Details of the Target
General Information of Target
| Target ID | LDTP07236 | |||||
|---|---|---|---|---|---|---|
| Target Name | Protein GPR107 (GPR107) | |||||
| Gene Name | GPR107 | |||||
| Gene ID | 57720 | |||||
| Synonyms |
KIAA1624; LUSTR1; Protein GPR107; Lung seven transmembrane receptor 1 |
|||||
| 3D Structure | ||||||
| Sequence |
MAALAPVGSPASRGPRLAAGLRLLPMLGLLQLLAEPGLGRVHHLALKDDVRHKVHLNTFG
FFKDGYMVVNVSSLSLNEPEDKDVTIGFSLDRTKNDGFSSYLDEDVNYCILKKQSVSVTL LILDISRSEVRVKSPPEAGTQLPKIIFSRDEKVLGQSQEPNVNPASAGNQTQKTQDGGKS KRSTVDSKAMGEKSFSVHNNGGAVSFQFFFNISTDDQEGLYSLYFHKCLGKELPSDKFTF SLDIEITEKNPDSYLSAGEIPLPKLYISMAFFFFLSGTIWIHILRKRRNDVFKIHWLMAA LPFTKSLSLVFHAIDYHYISSQGFPIEGWAVVYYITHLLKGALLFITIALIGTGWAFIKH ILSDKDKKIFMIVIPLQVLANVAYIIIESTEEGTTEYGLWKDSLFLVDLLCCGAILFPVV WSIRHLQEASATDGKGDSMGPLQQRANLRAGSRIESHHFAQADLELLASSCPPASVSQRA GITAAINLAKLKLFRHYYVLIVCYIYFTRIIAFLLKLAVPFQWKWLYQLLDETATLVFFV LTGYKFRPASDNPYLQLSQEEEDLEMESVVTTSGVMESMKKVKKVTNGSVEPQGEWEGAV |
|||||
| Target Bioclass |
Transporter and channel
|
|||||
| Family |
LU7TM family
|
|||||
| Subcellular location |
Cell membrane
|
|||||
| Function |
Has been proposed to act as a receptor for neuronostatin, a peptide derived from the somatostatin/SST precursor. Involved in blood sugar regulation through the induction of glucagon in response to low glucose.; (Microbial infection) Required for intoxication by Pseudomonas aeruginosa exotoxin A and Campylobacter jejuni CDT. May contribute to the retrograde transport of bacterial toxins, including cholera toxin, from the trans-Golgi network to the endoplasmic reticulum.
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
| ChEMBL ID | ||||||
Probe(s) Labeling This Target
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
|
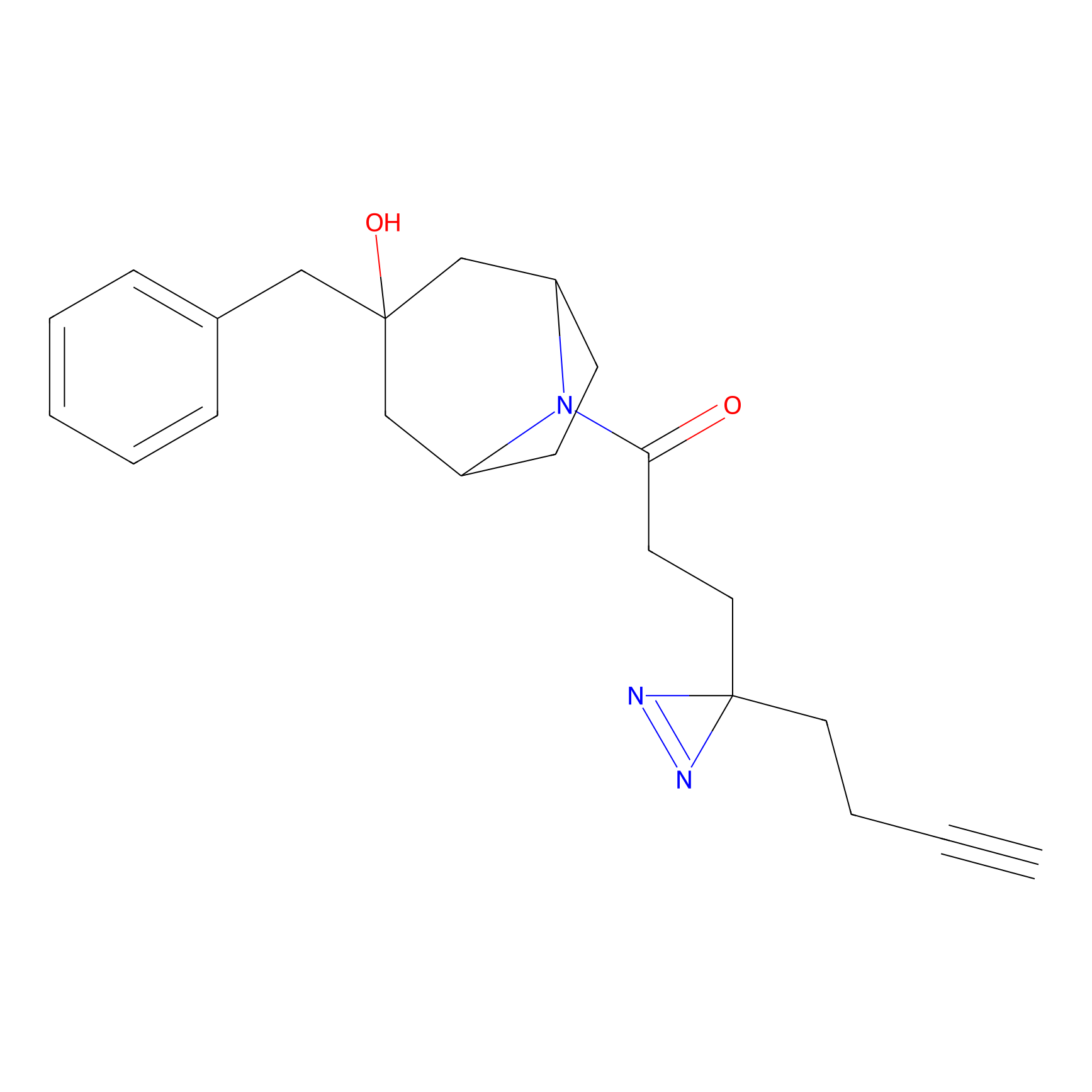
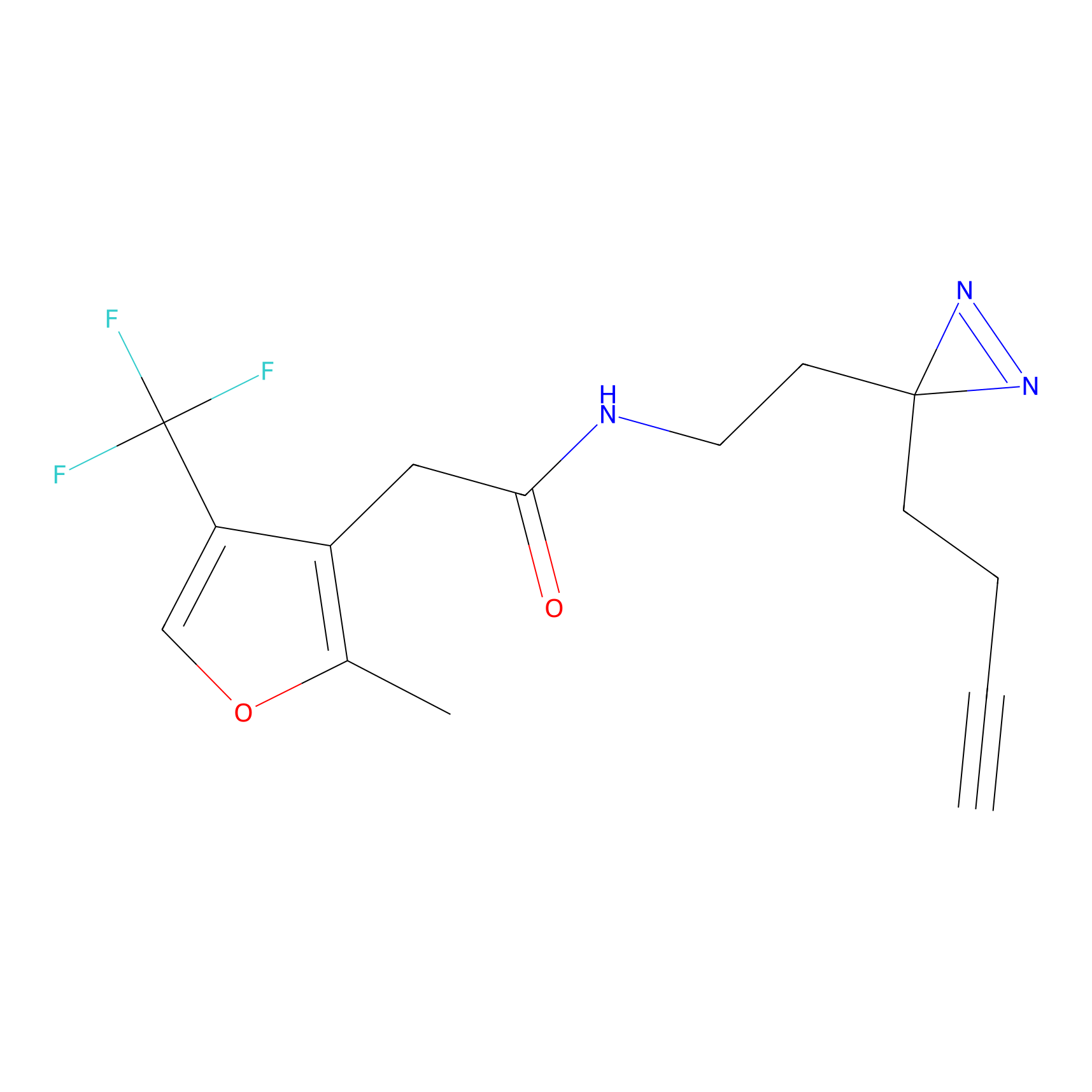
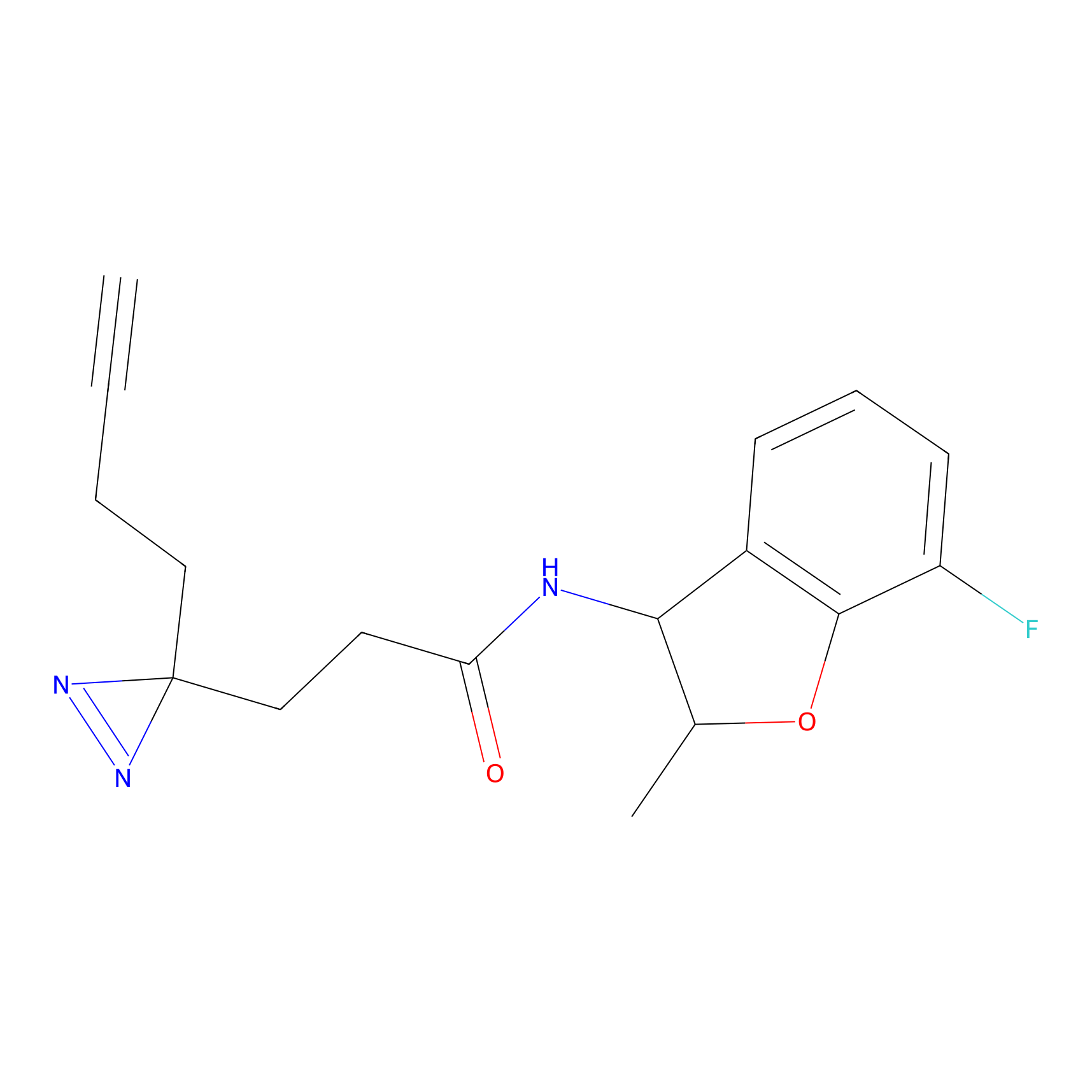
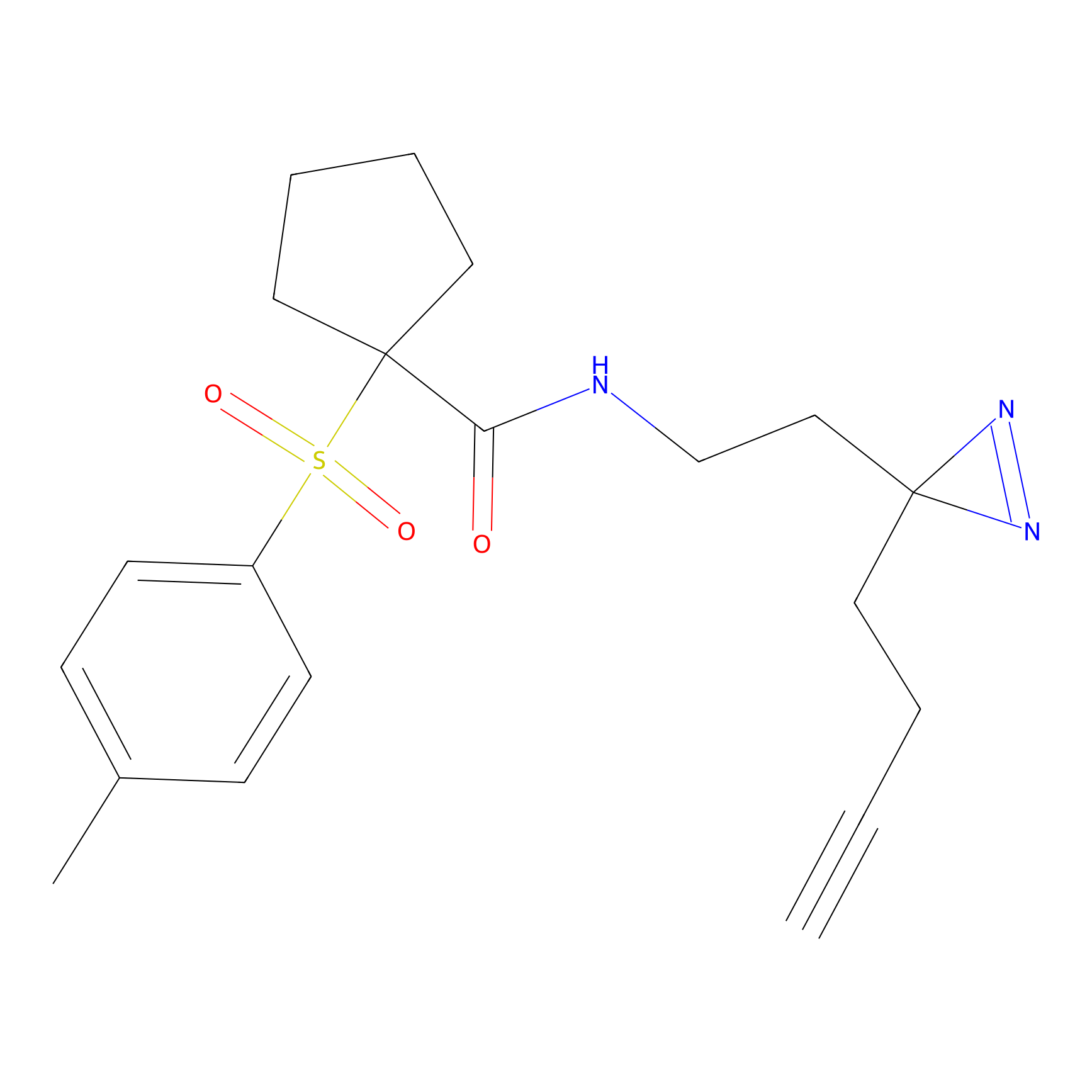
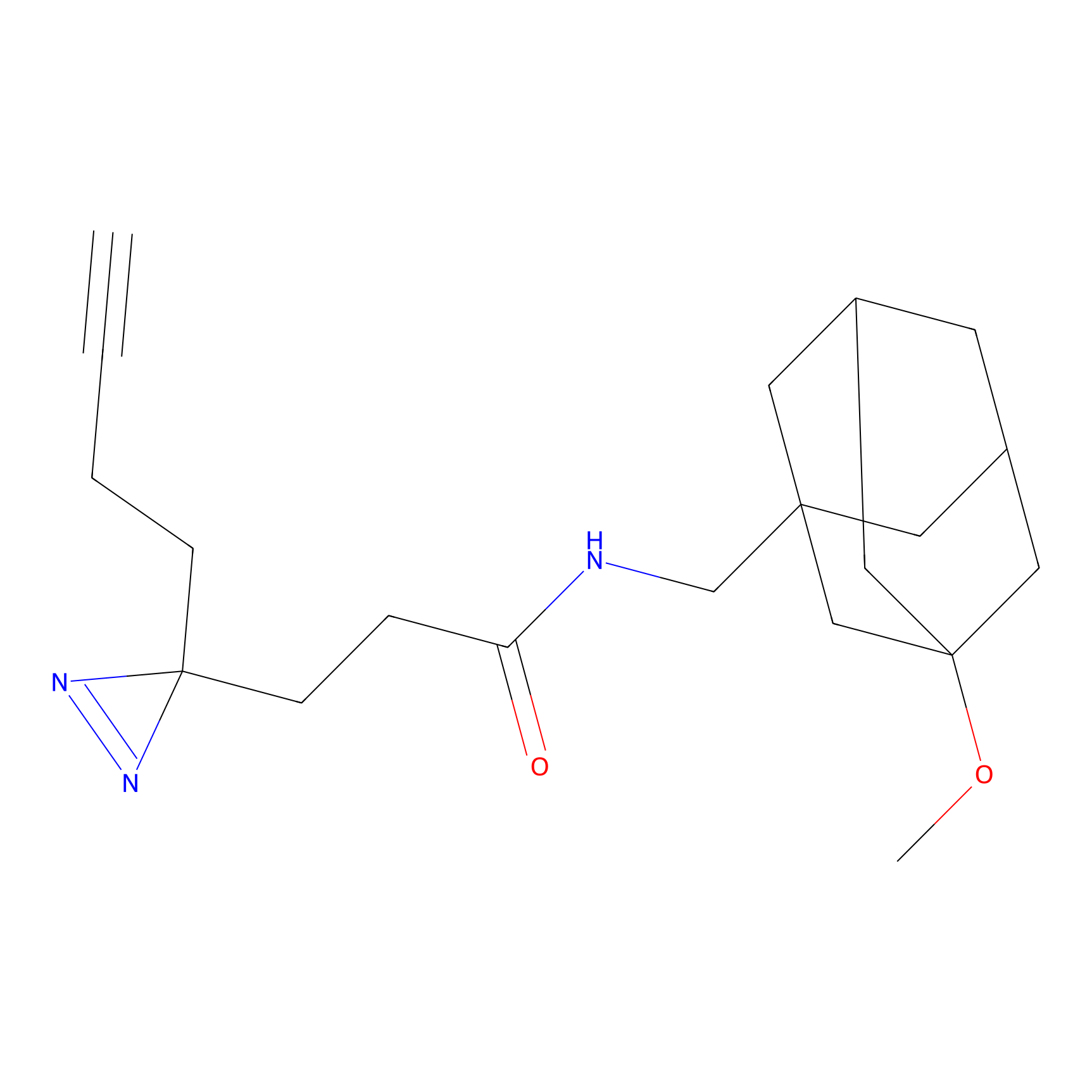
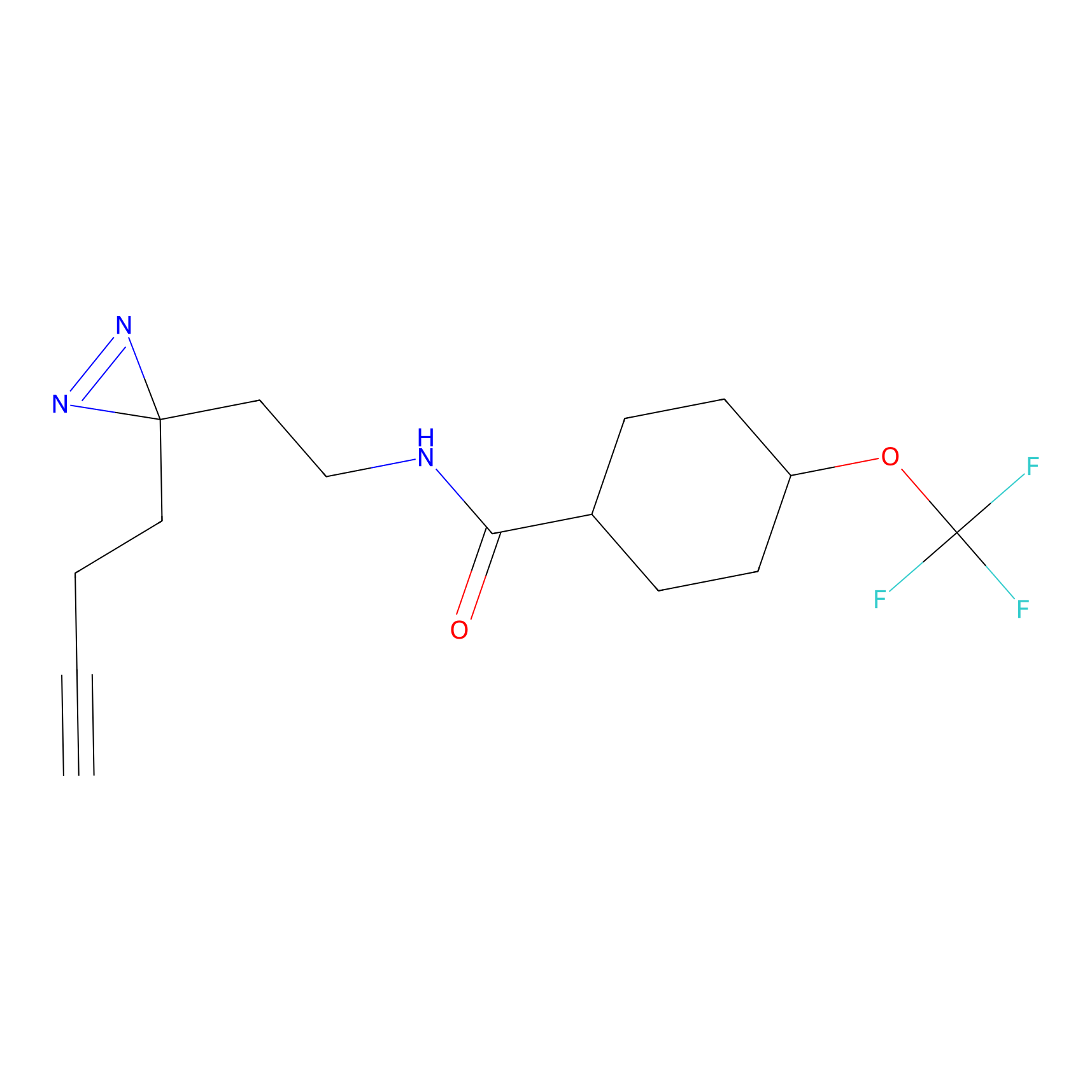
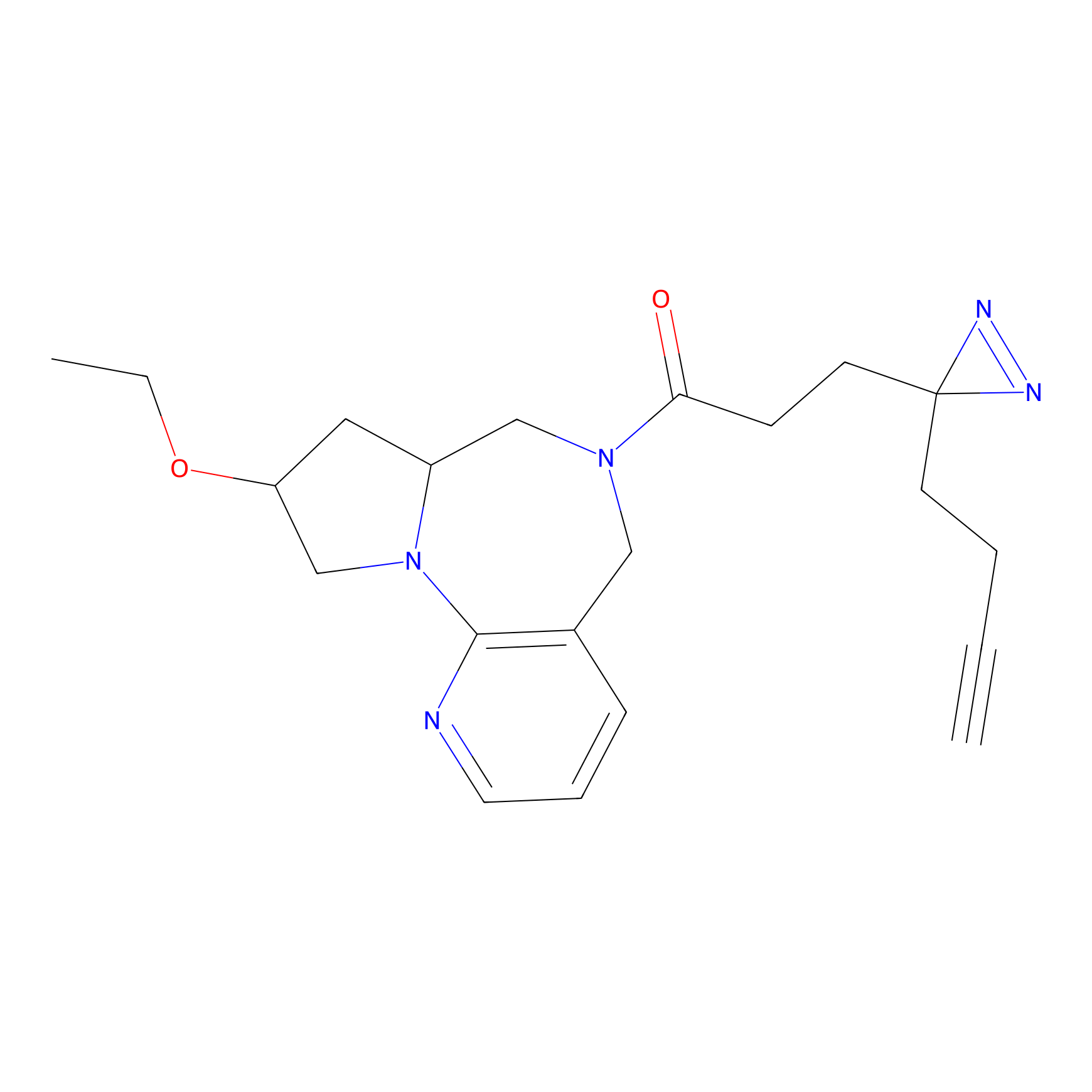
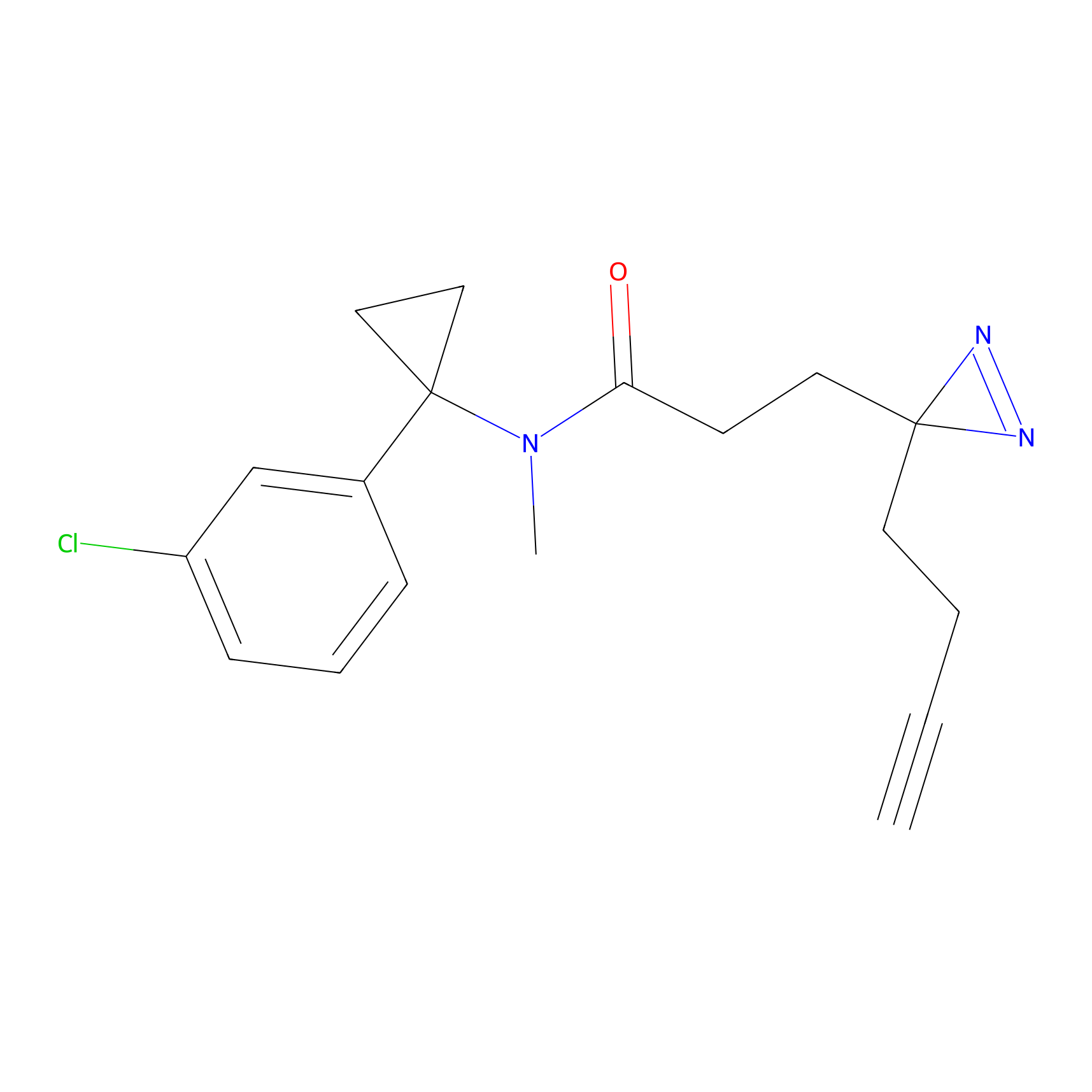
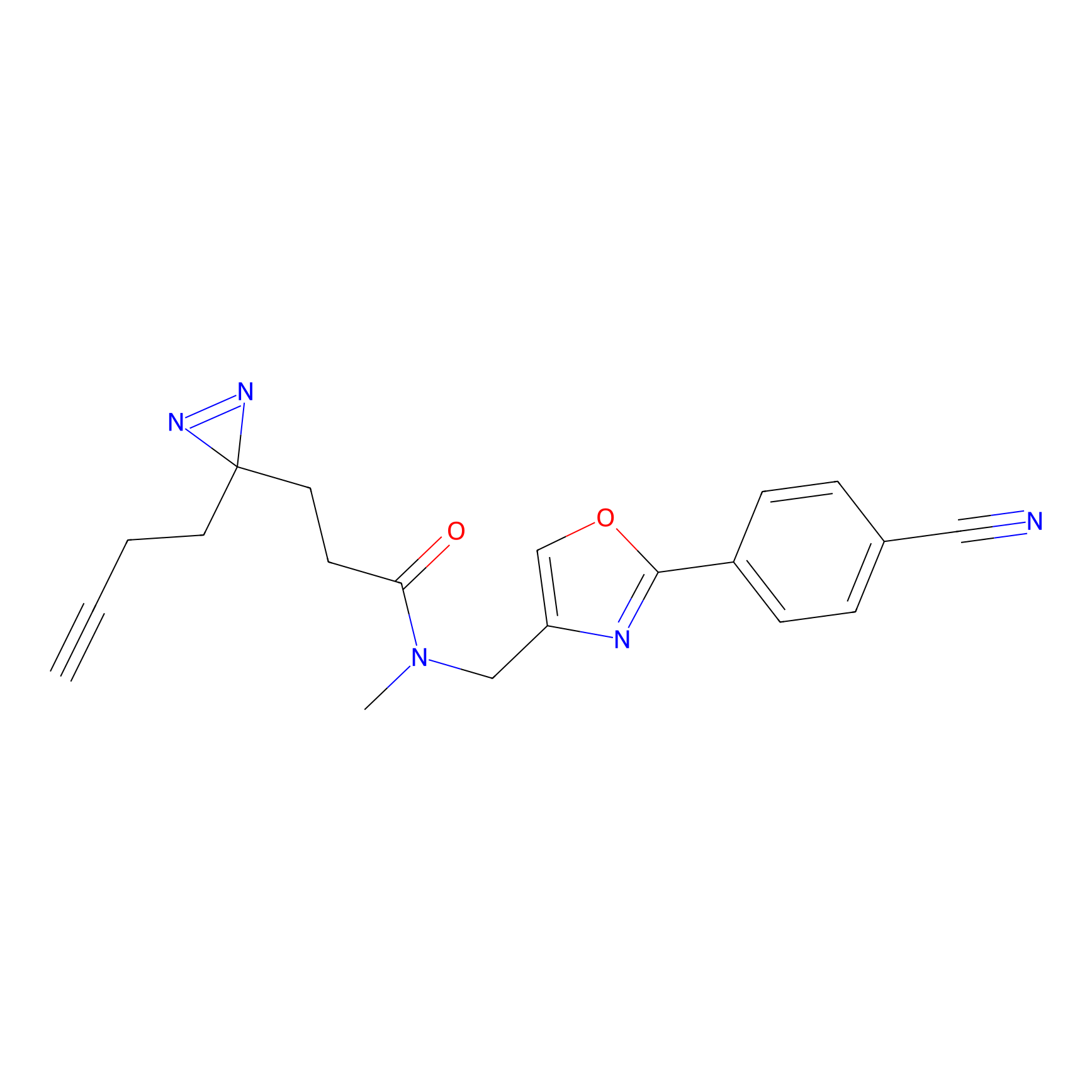
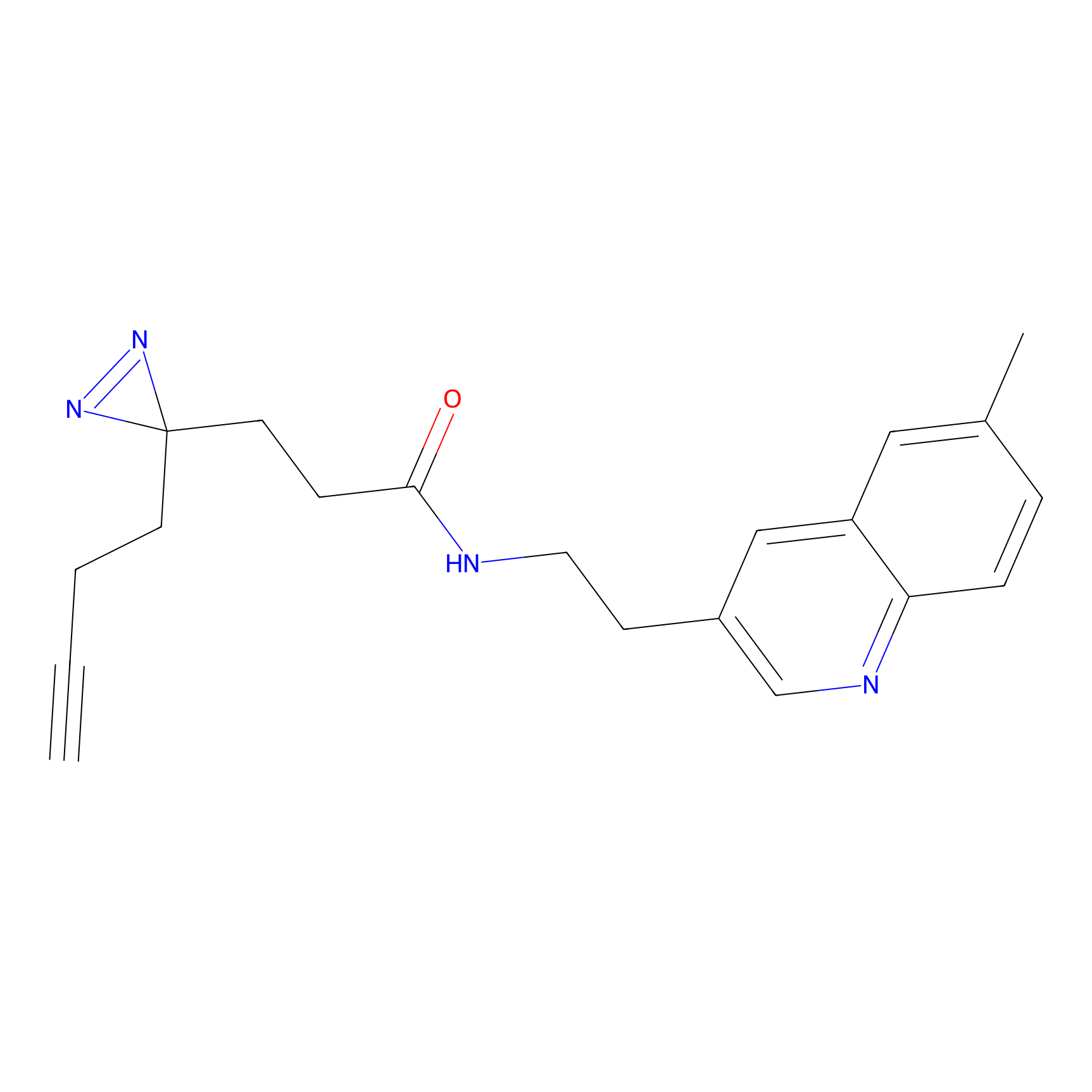
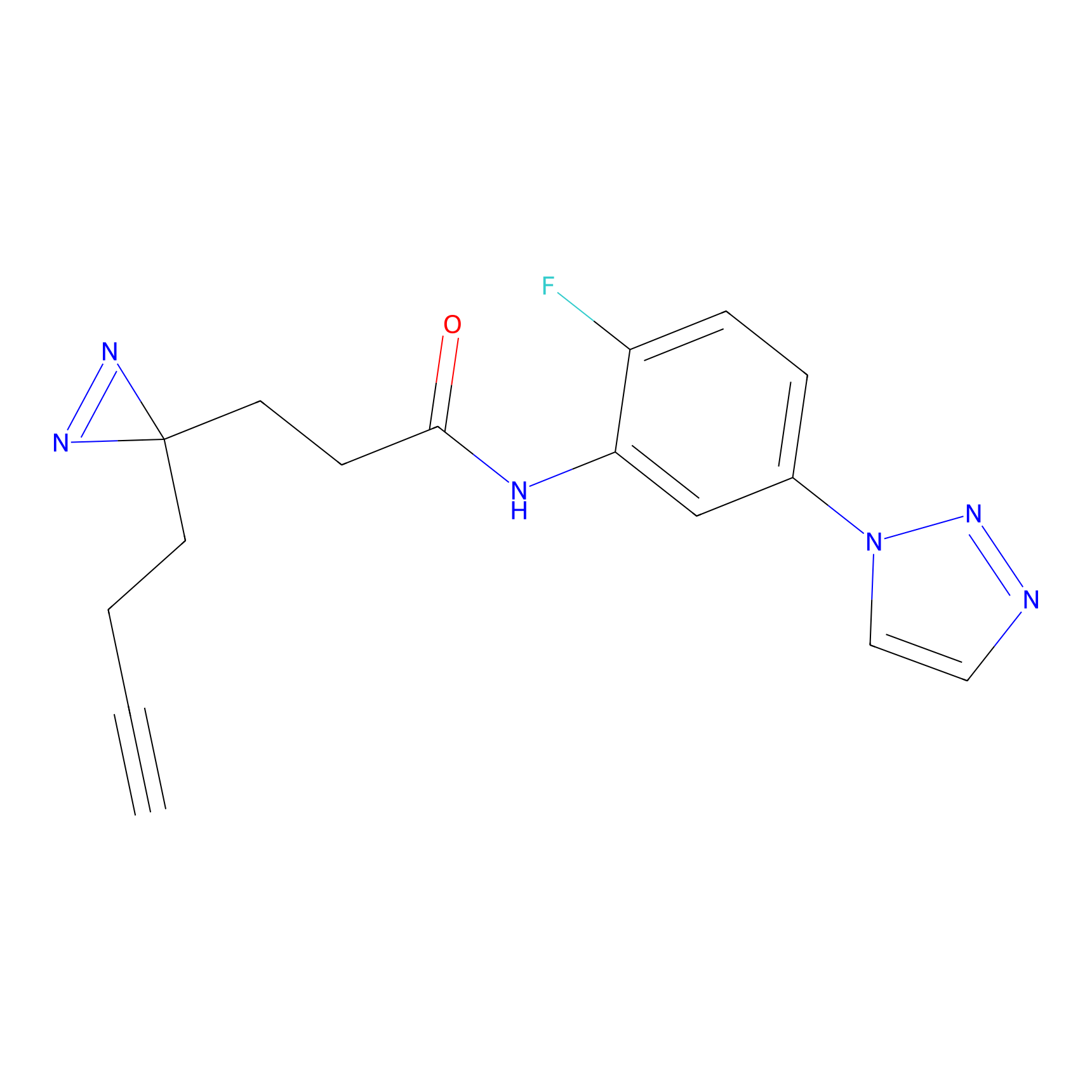
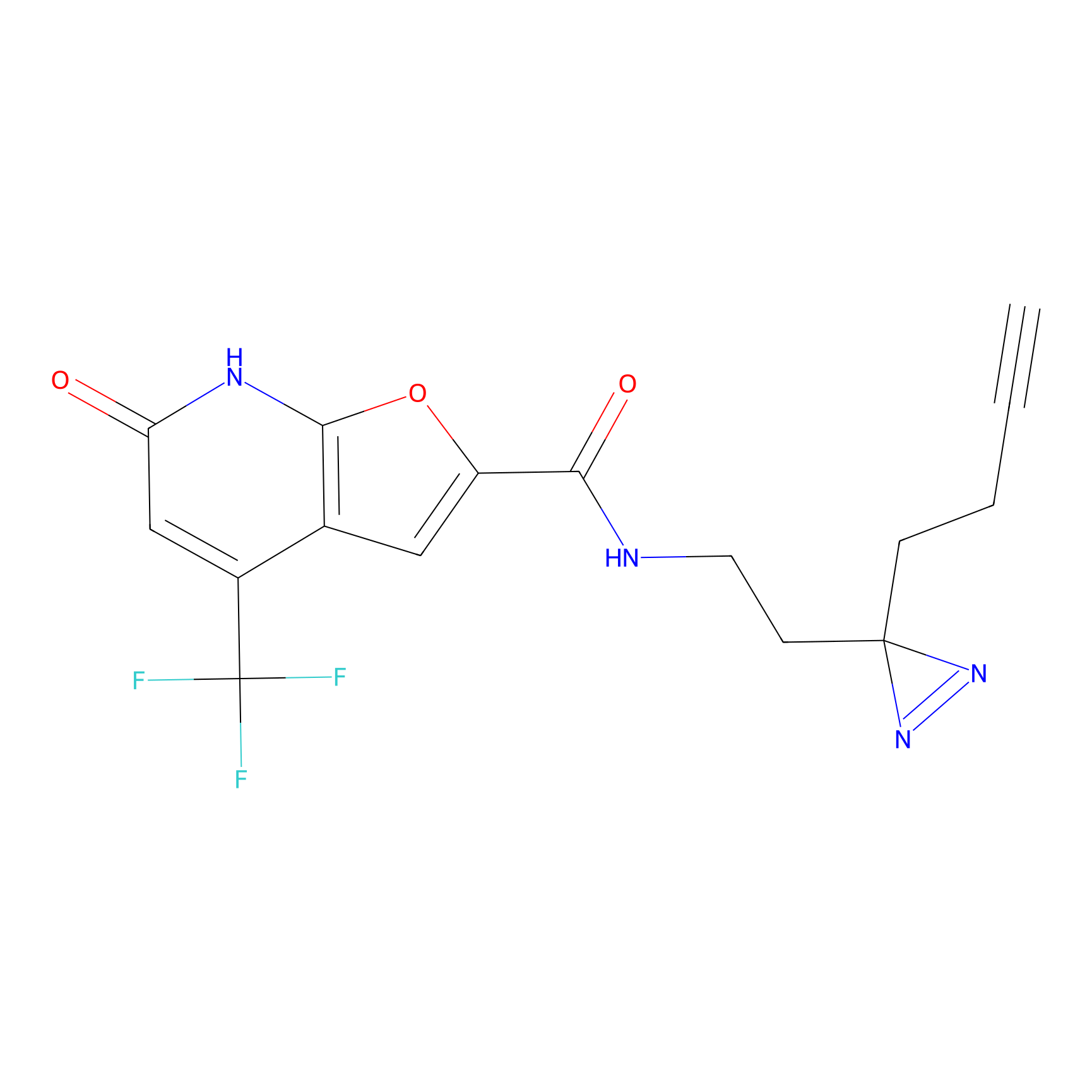
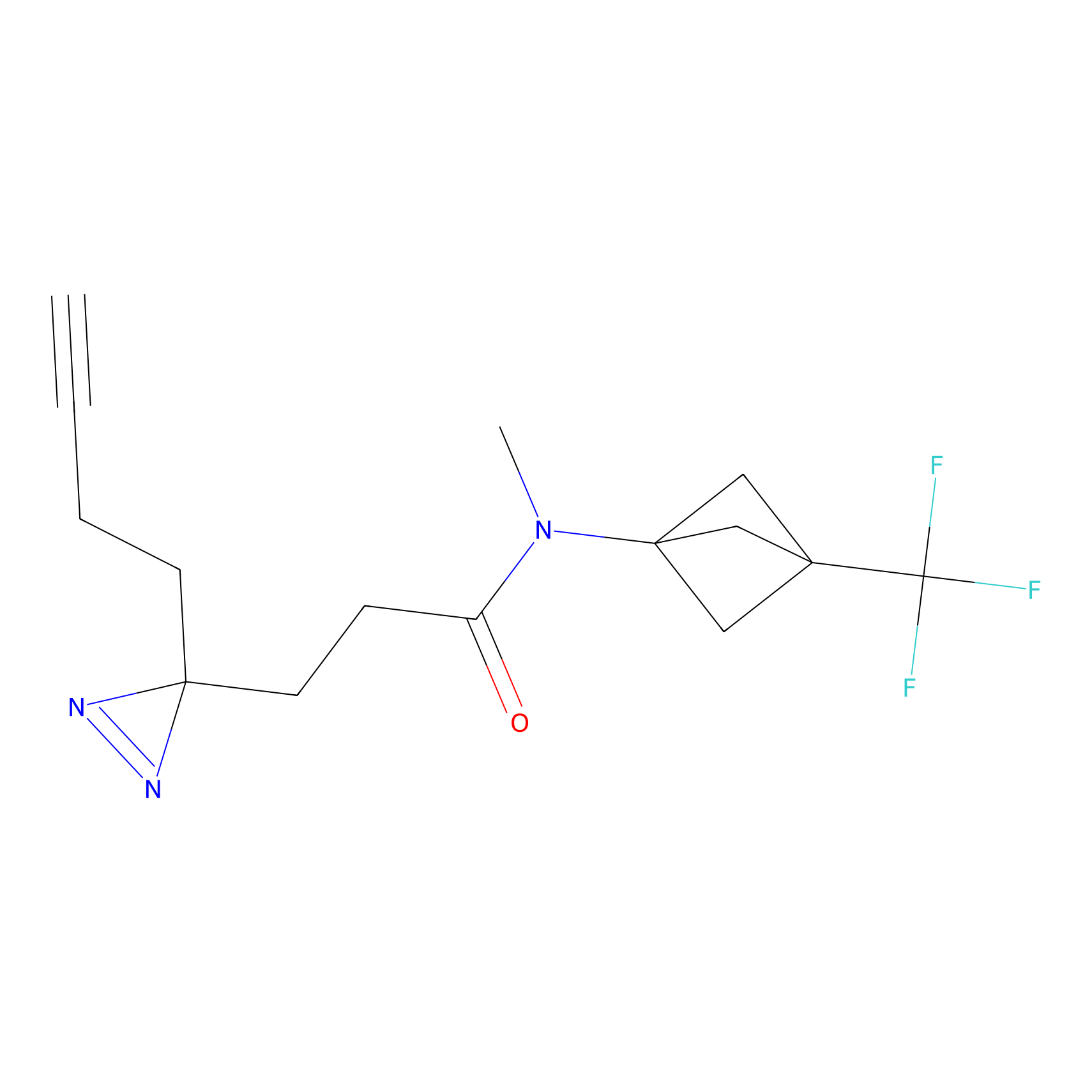
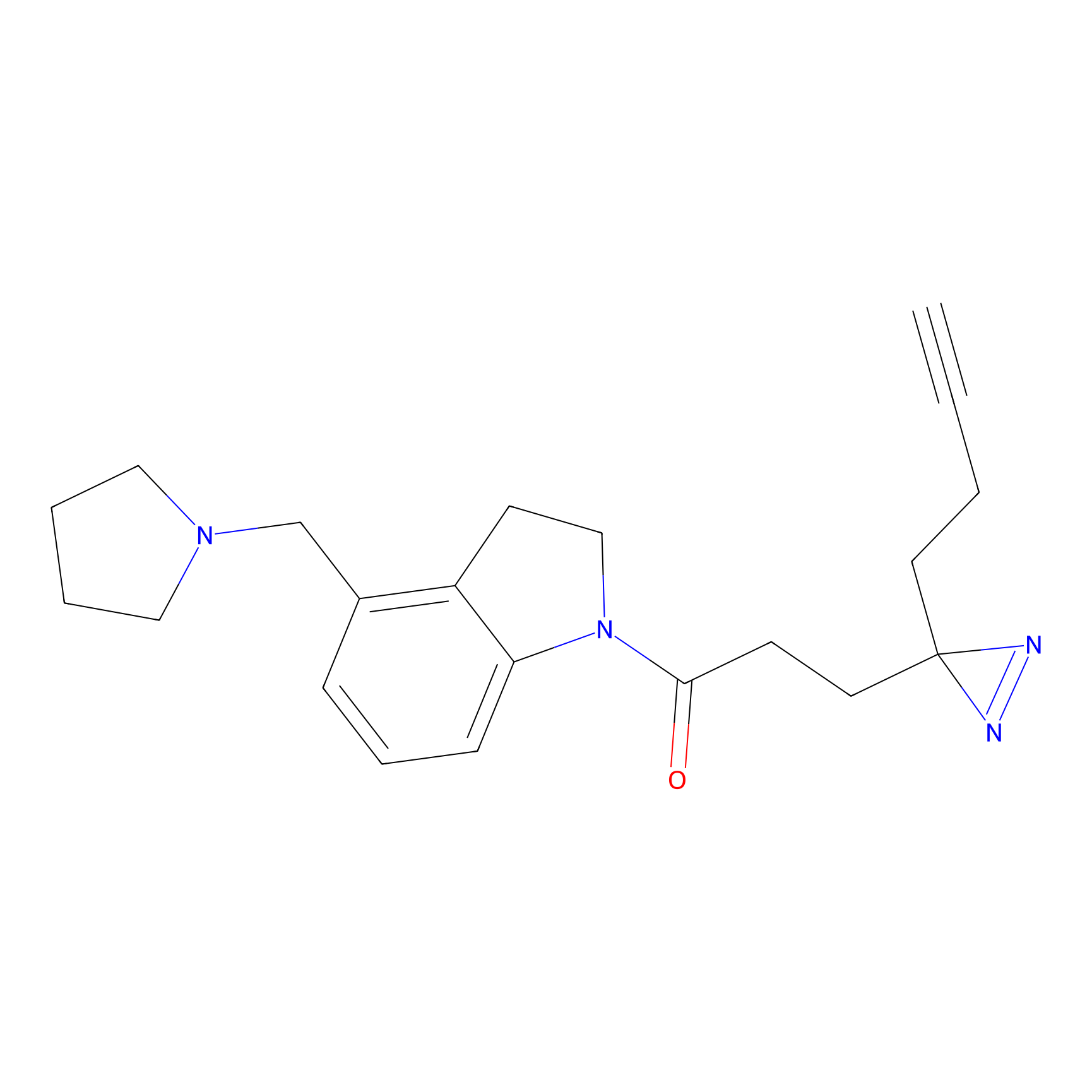
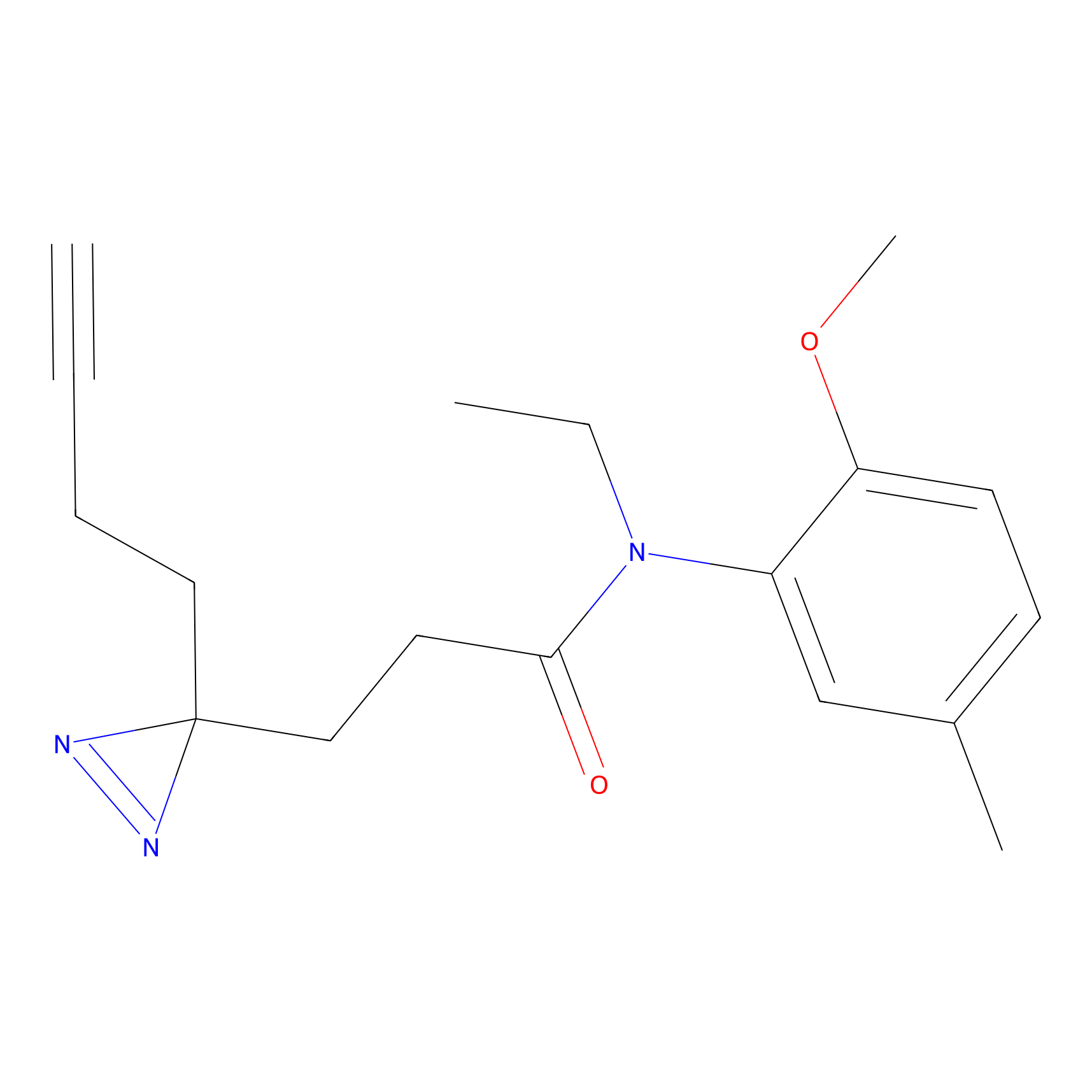
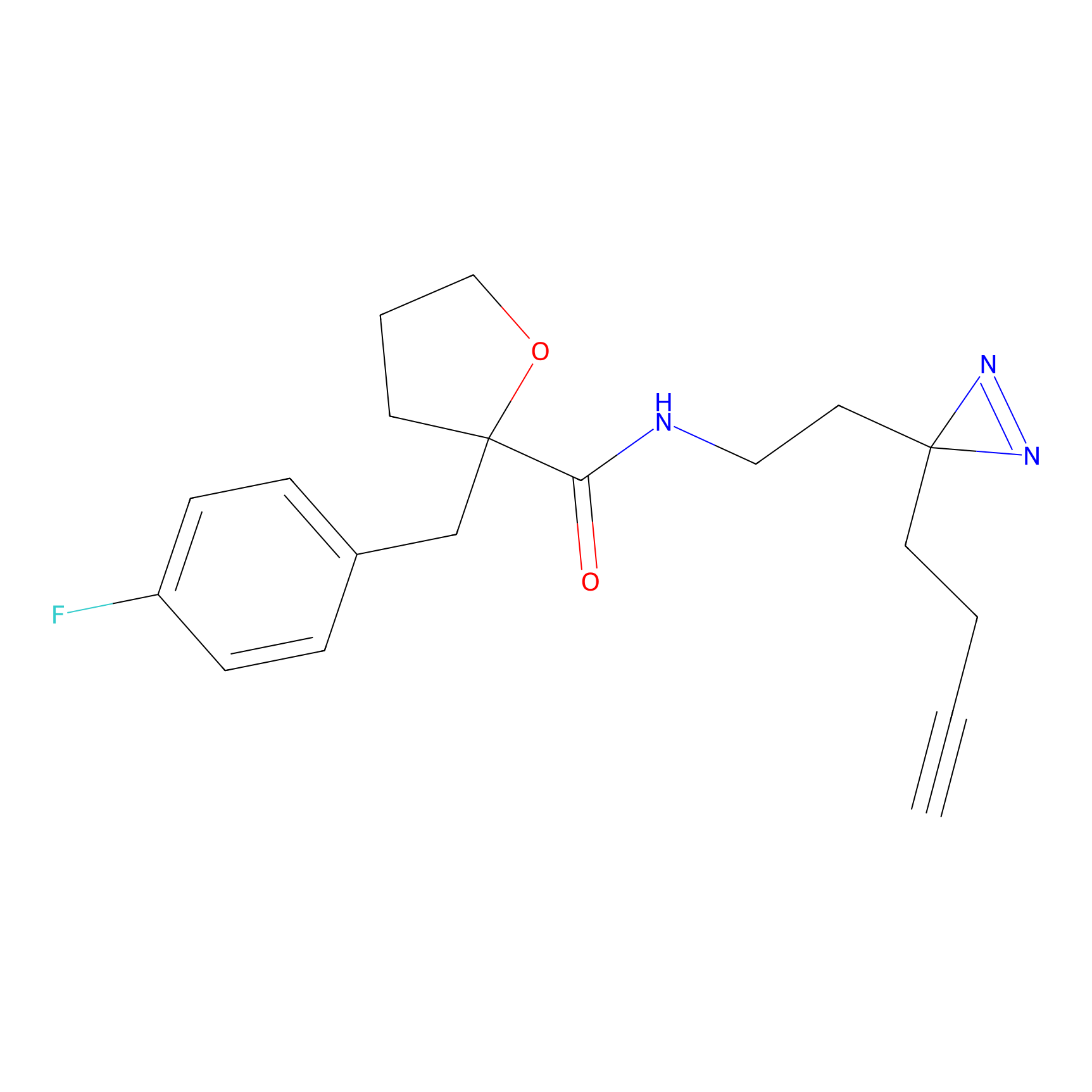
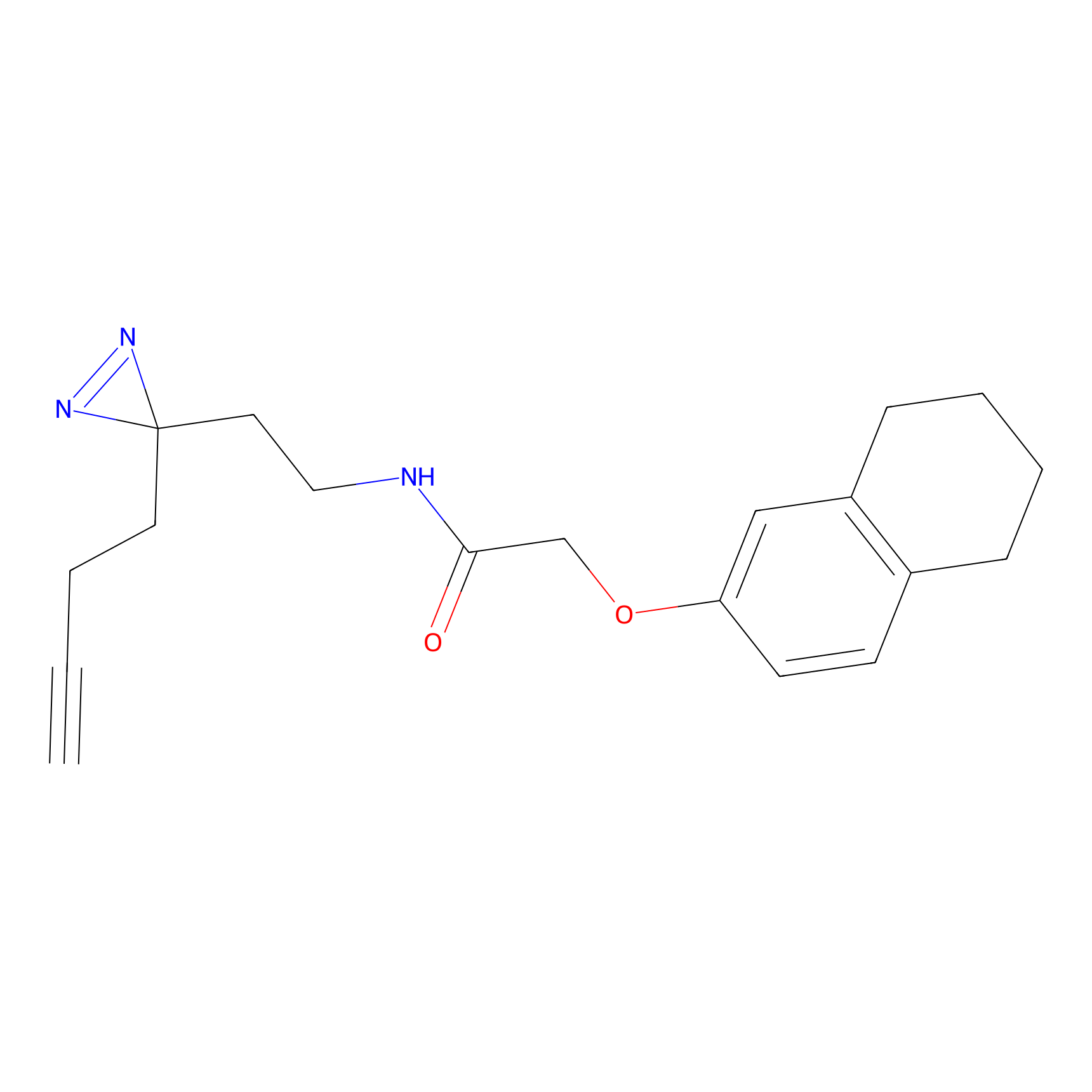
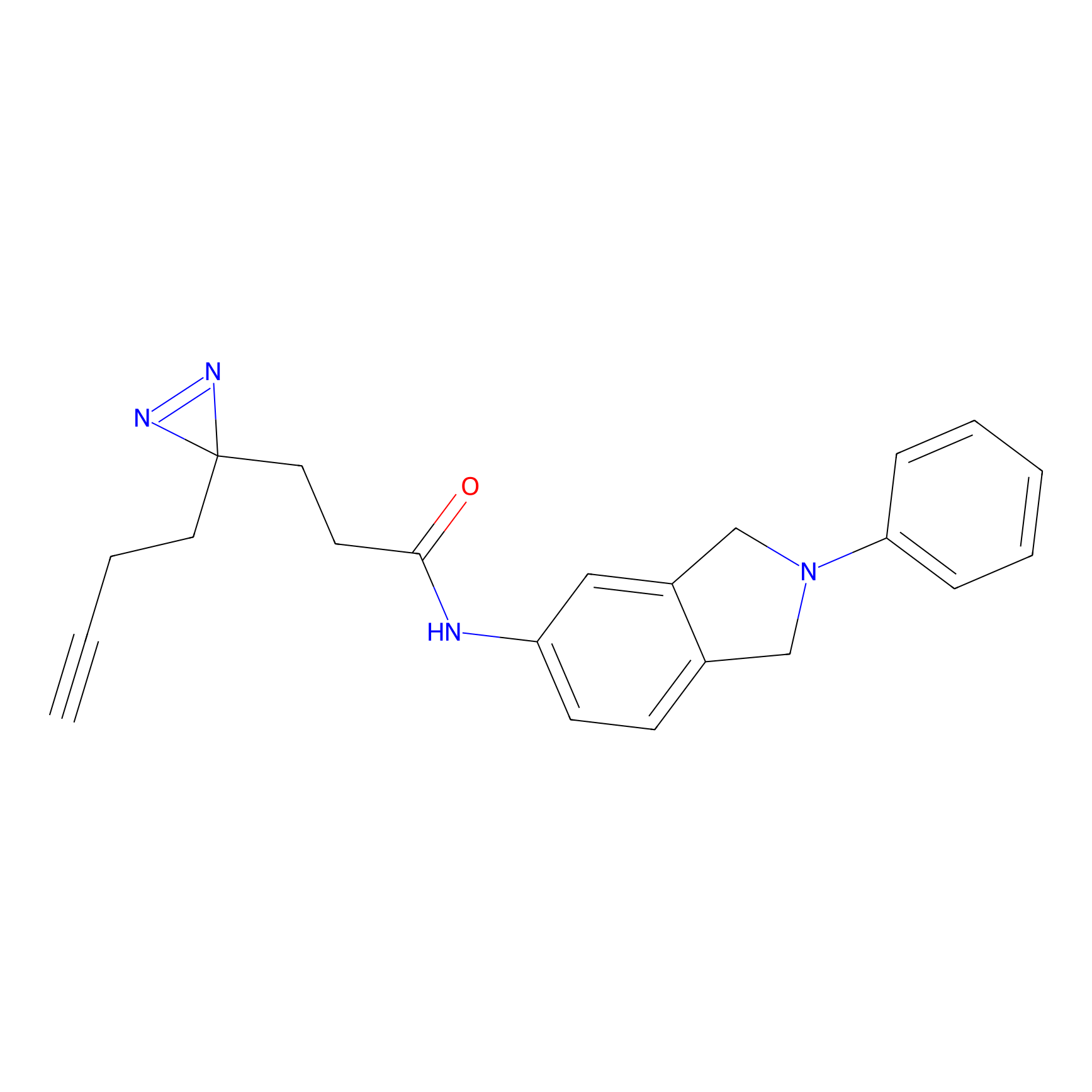
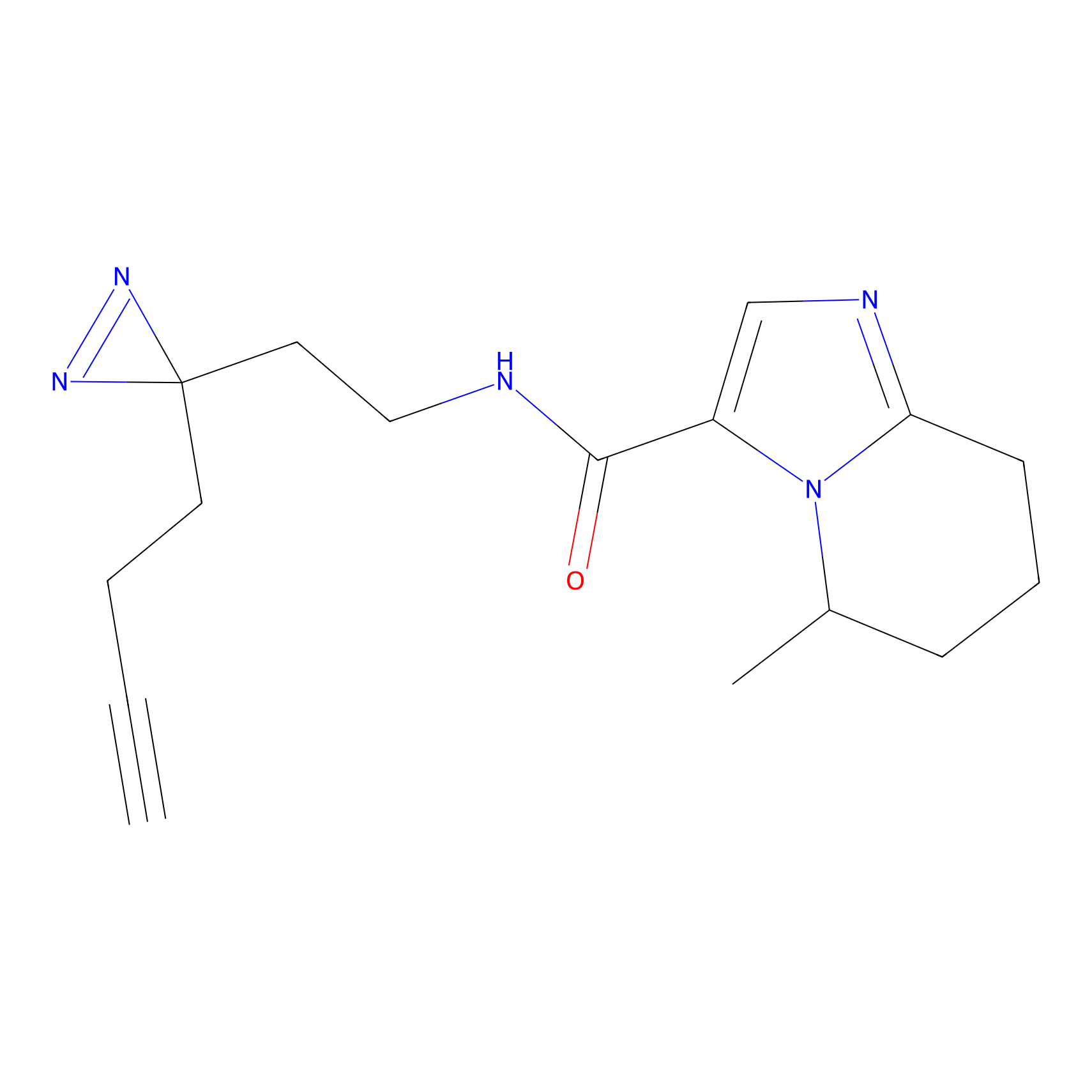
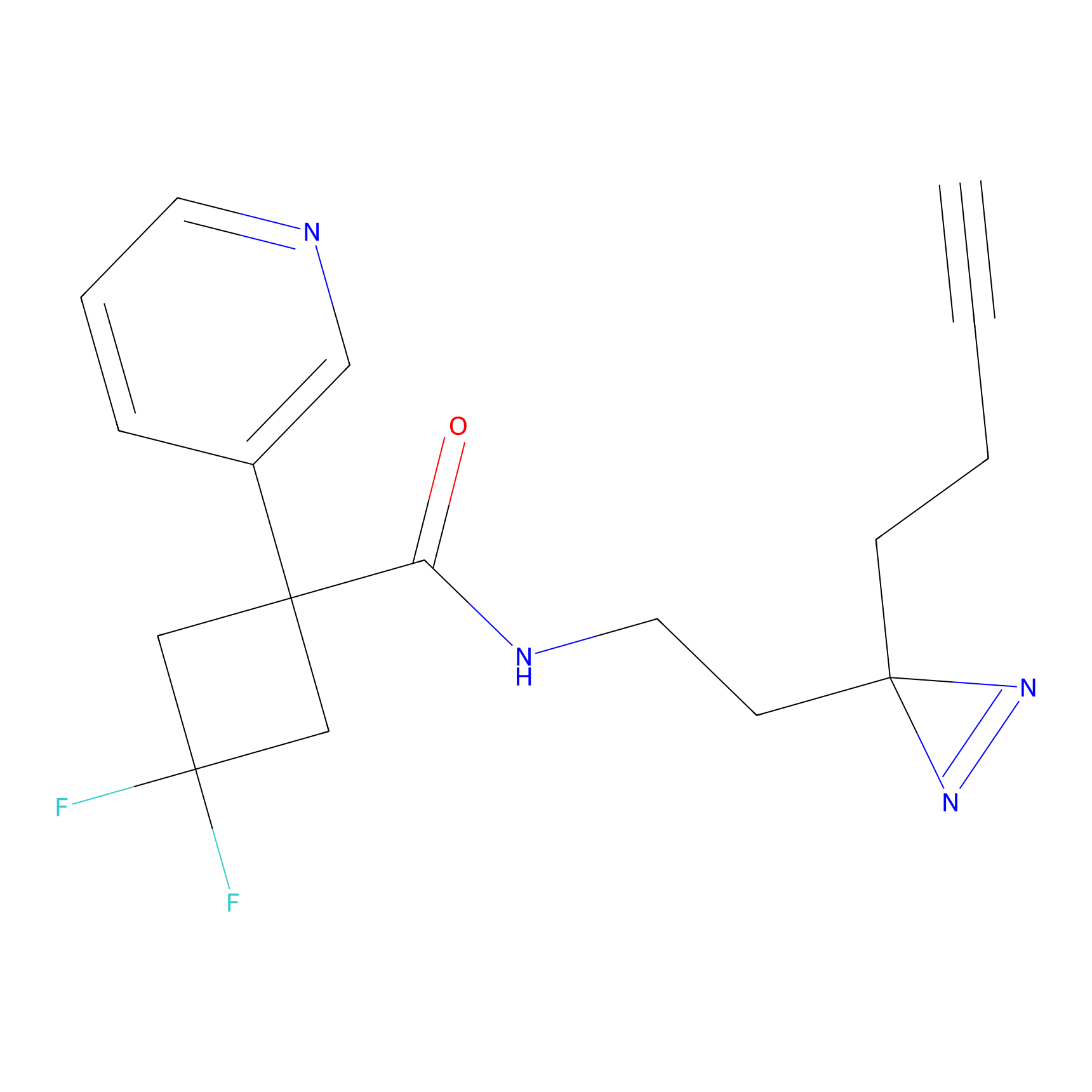
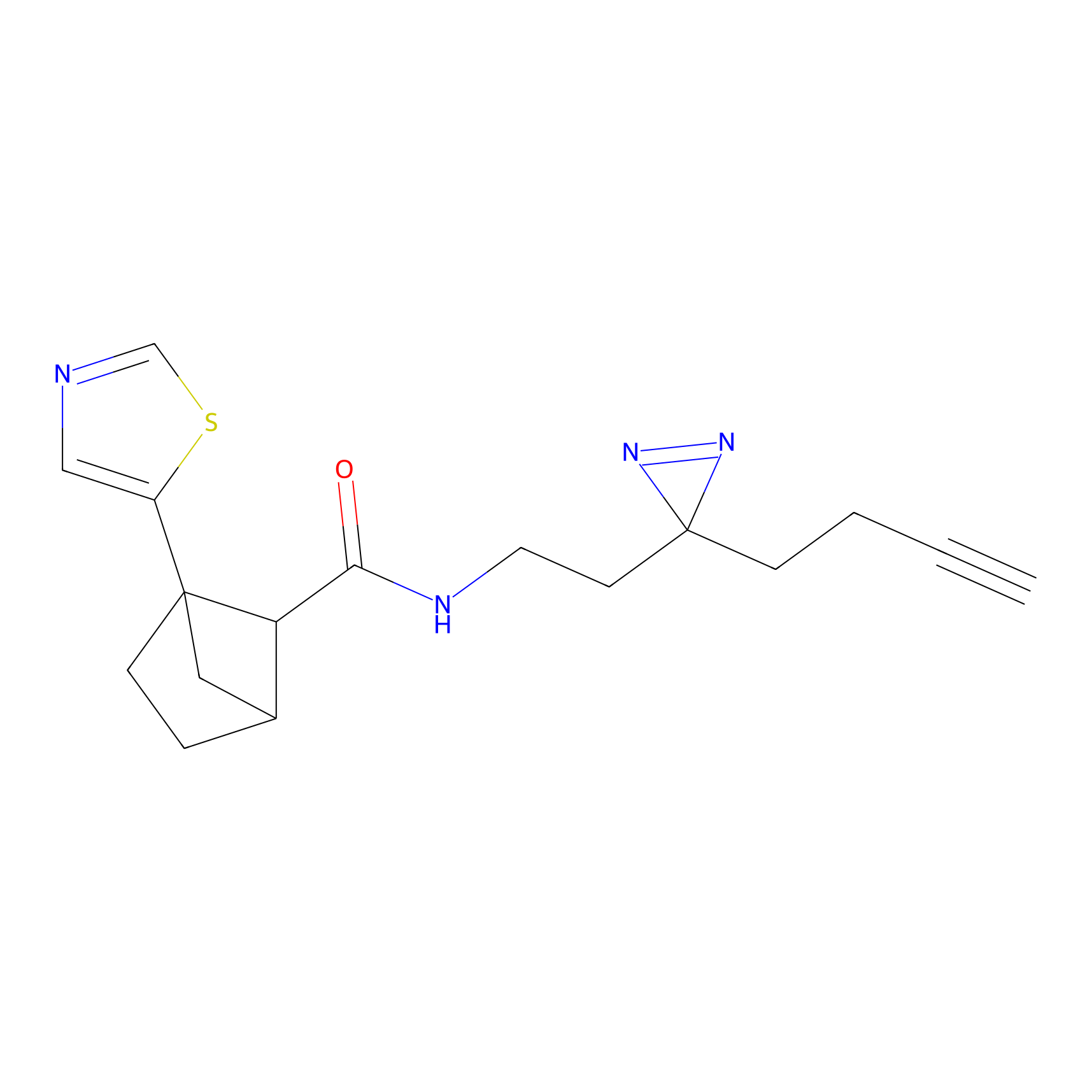
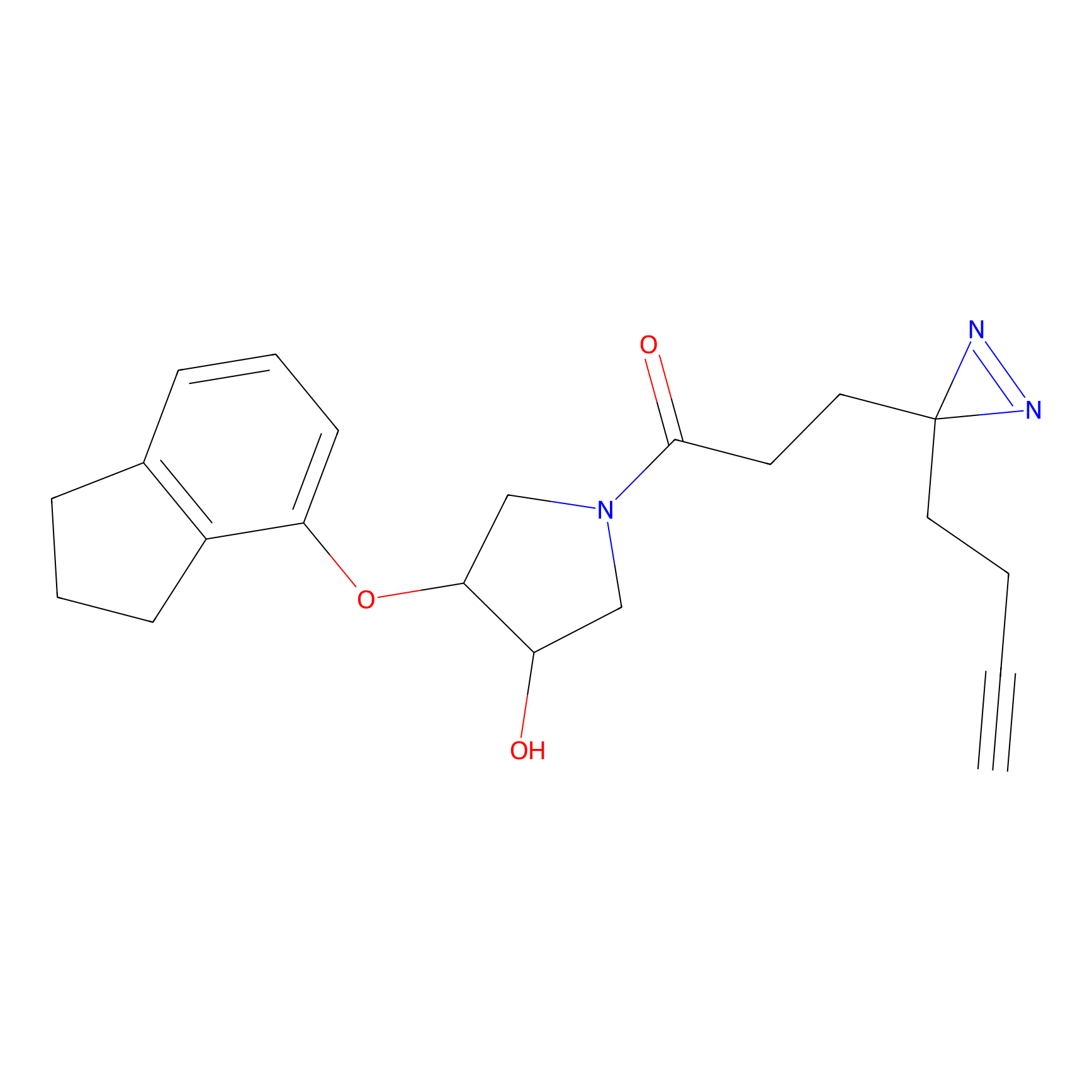
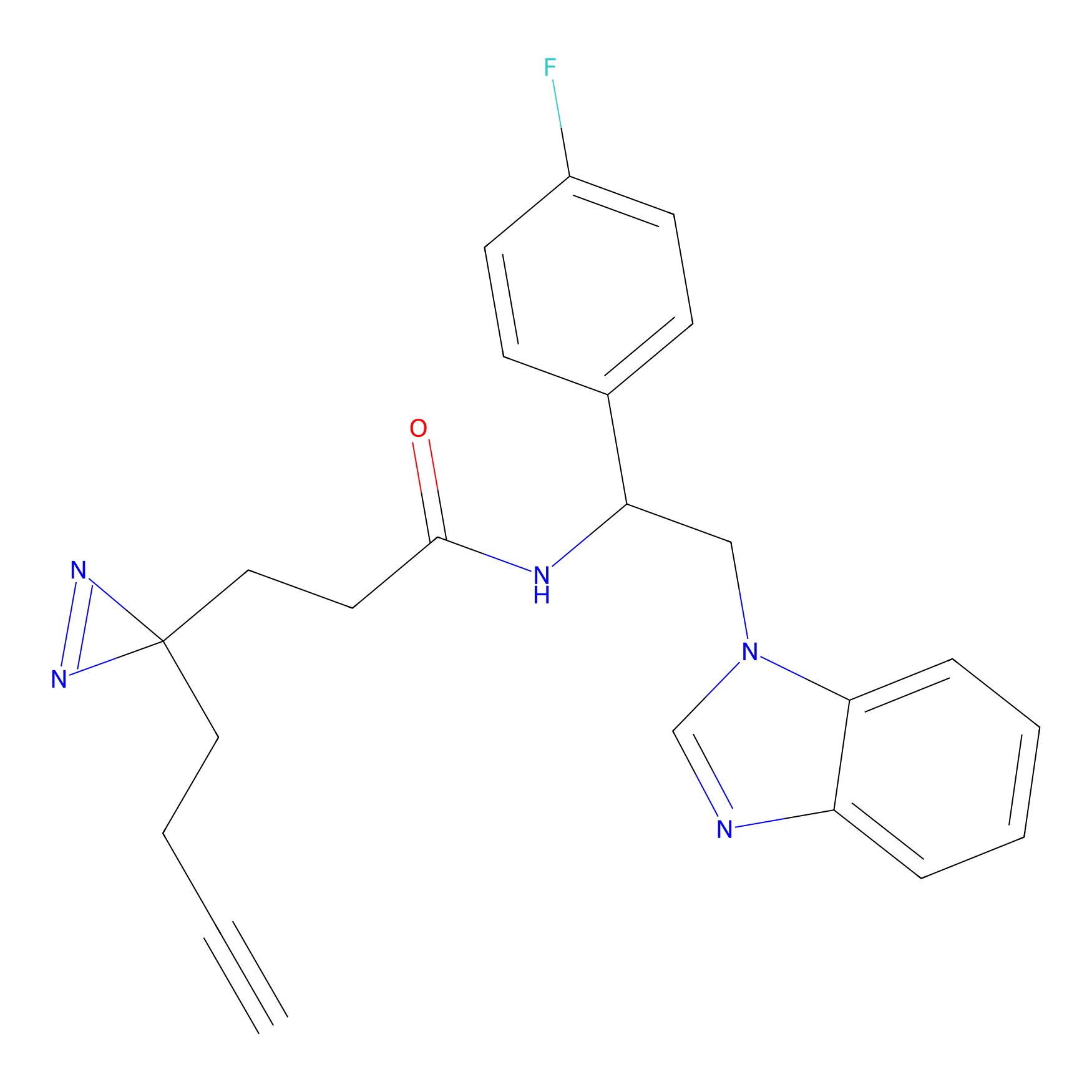
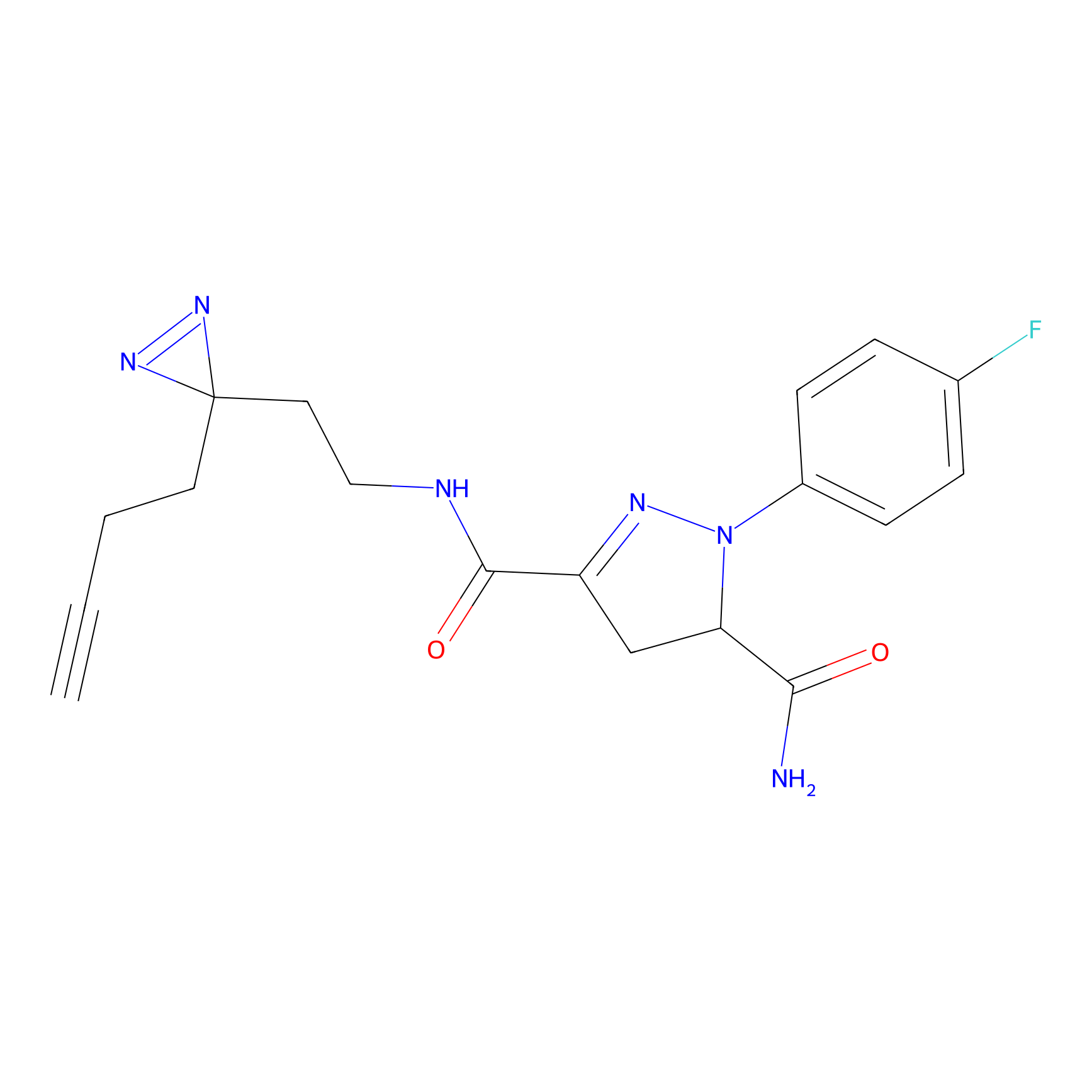
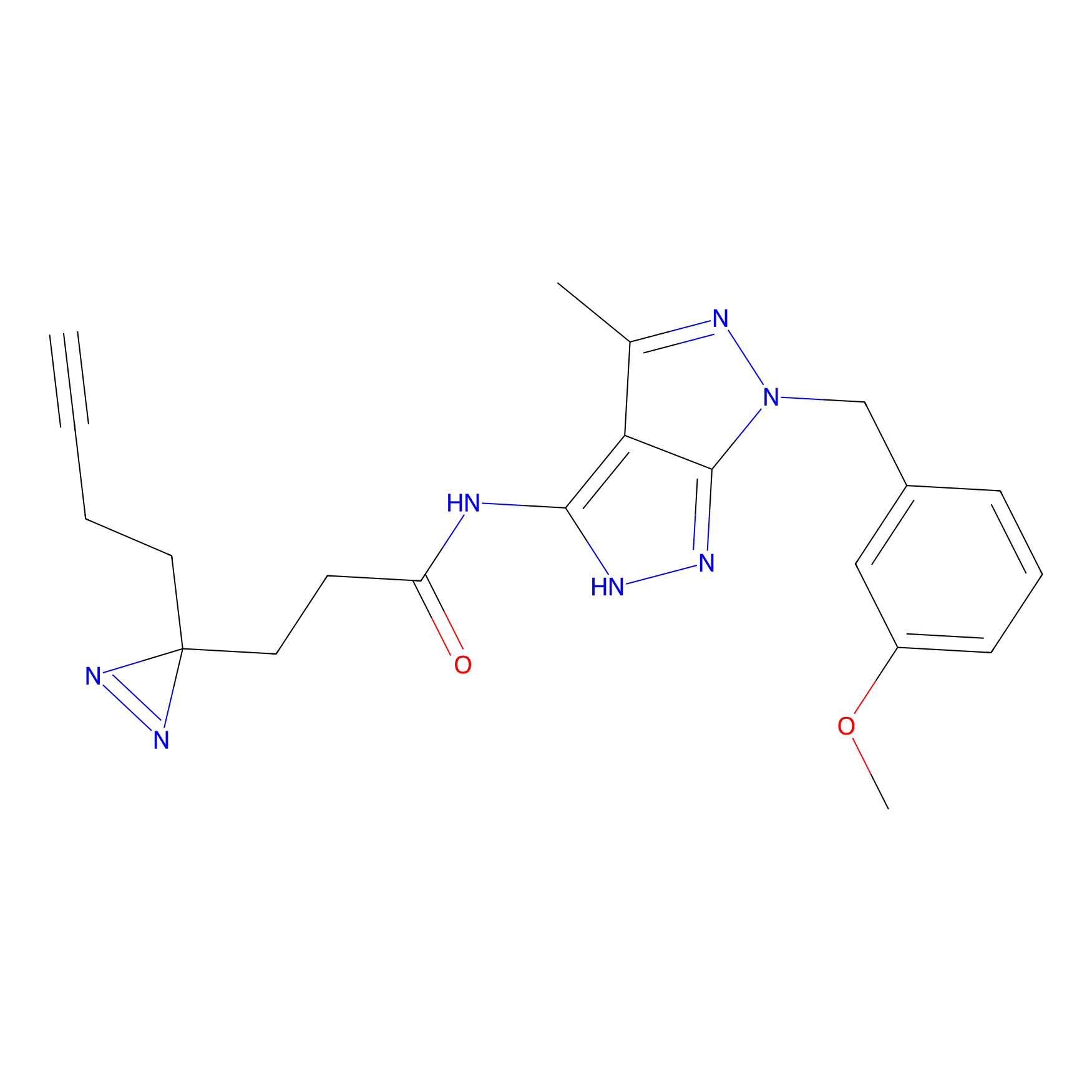
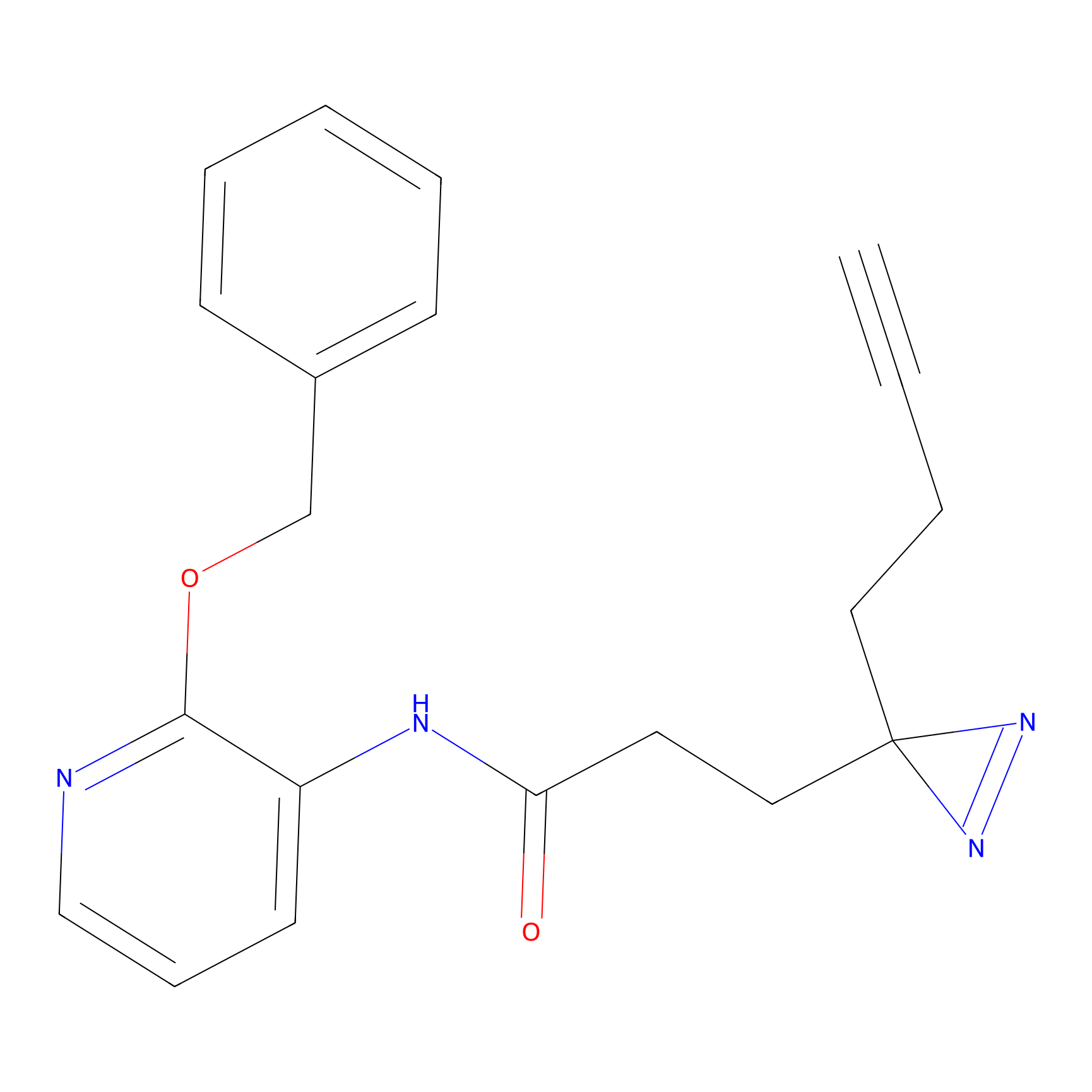
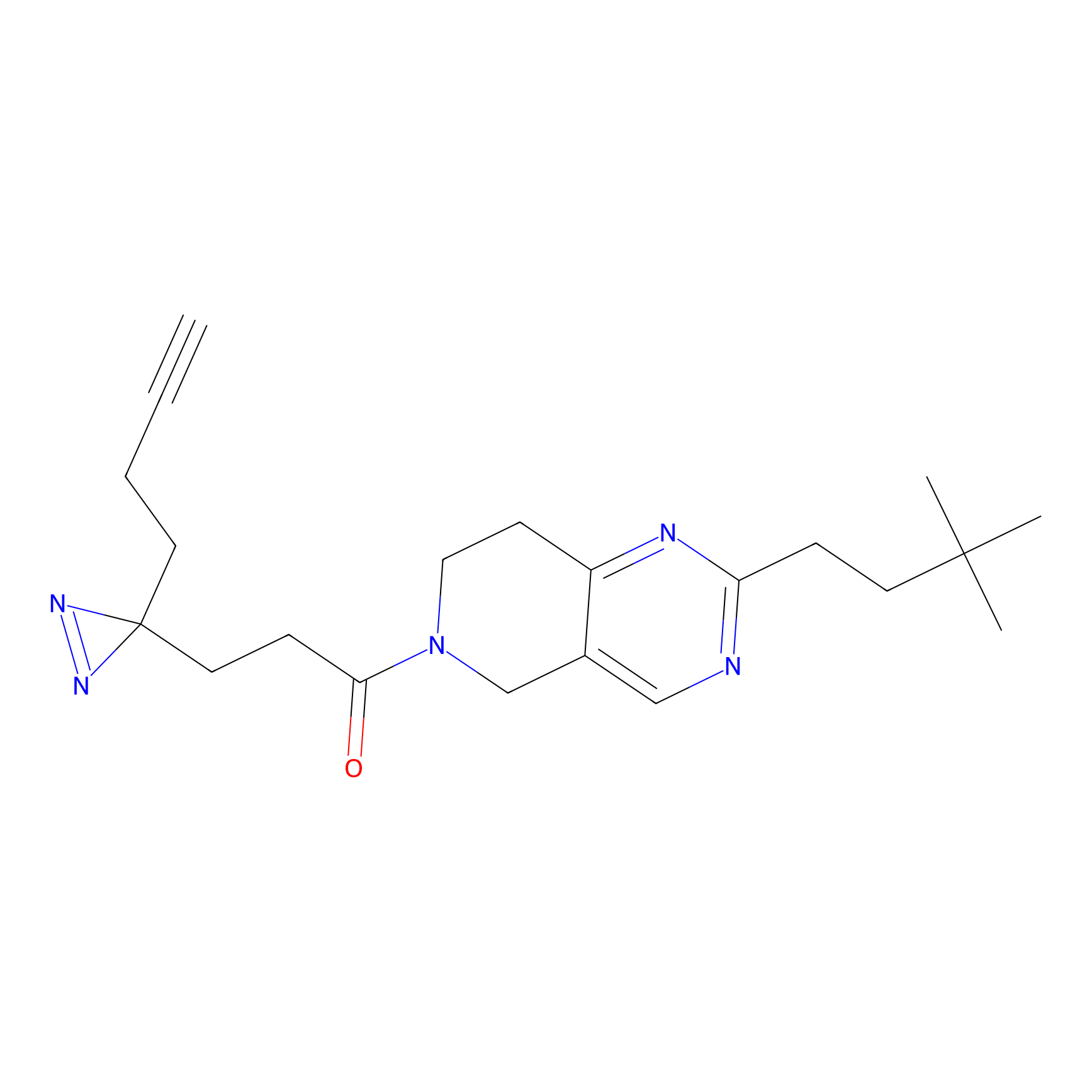
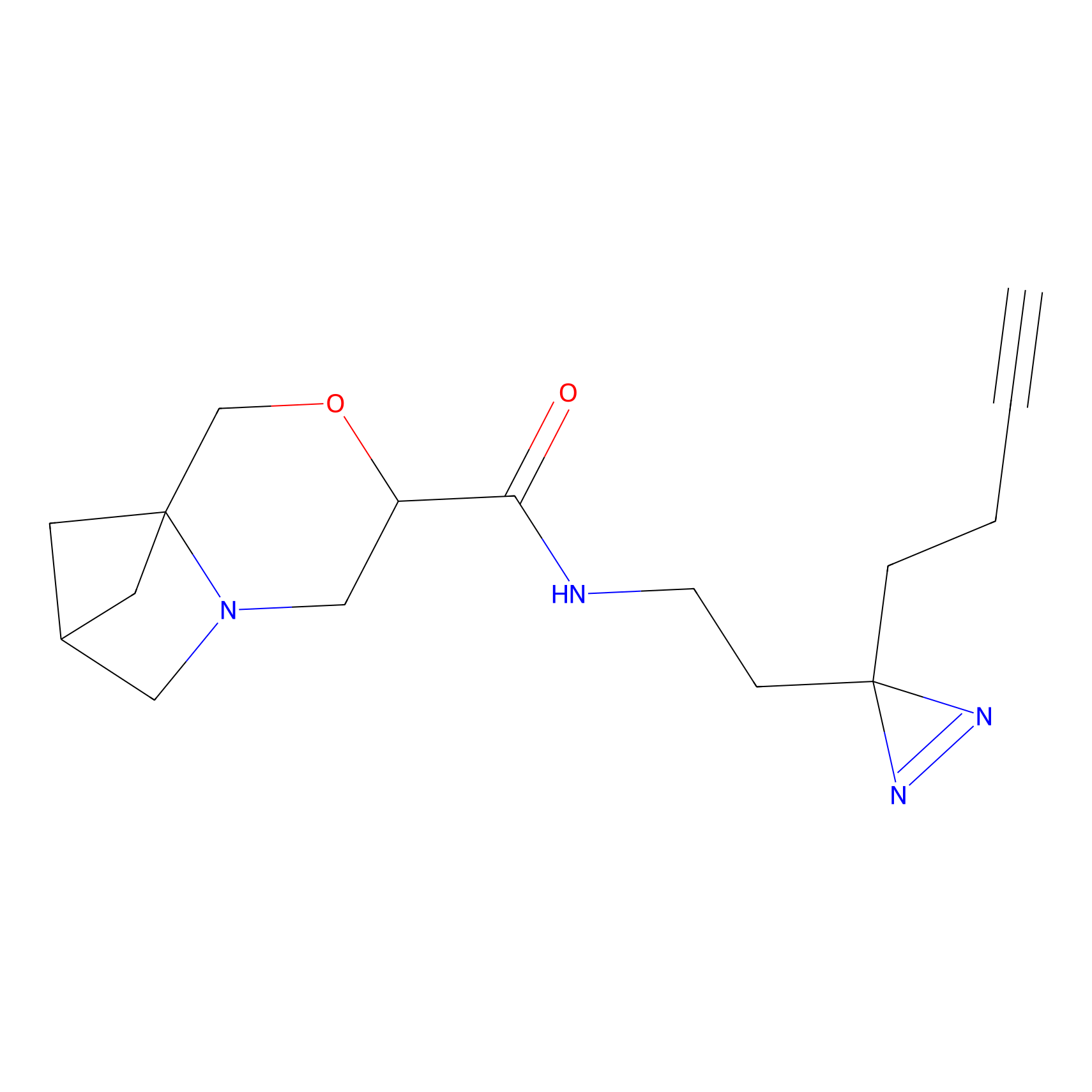
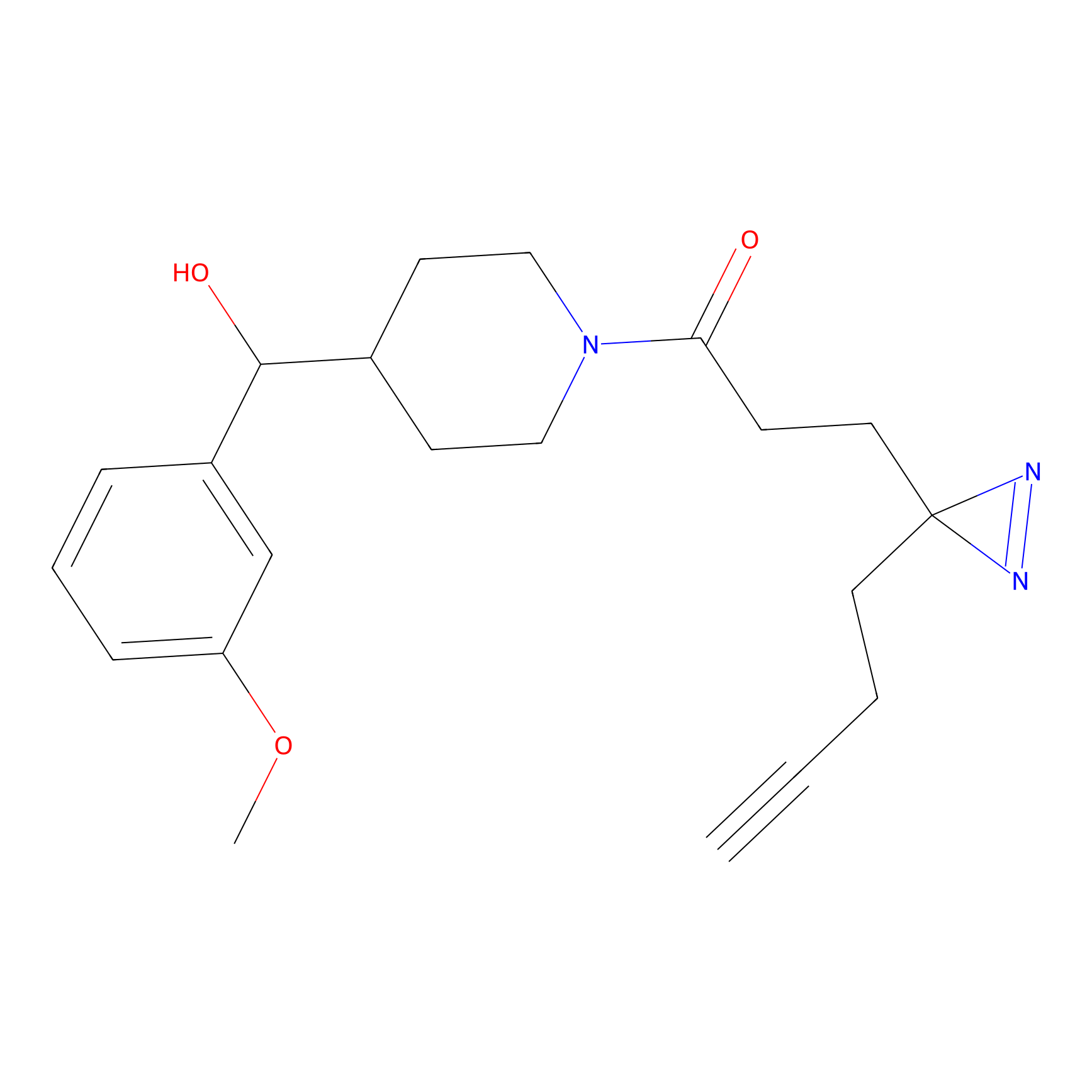
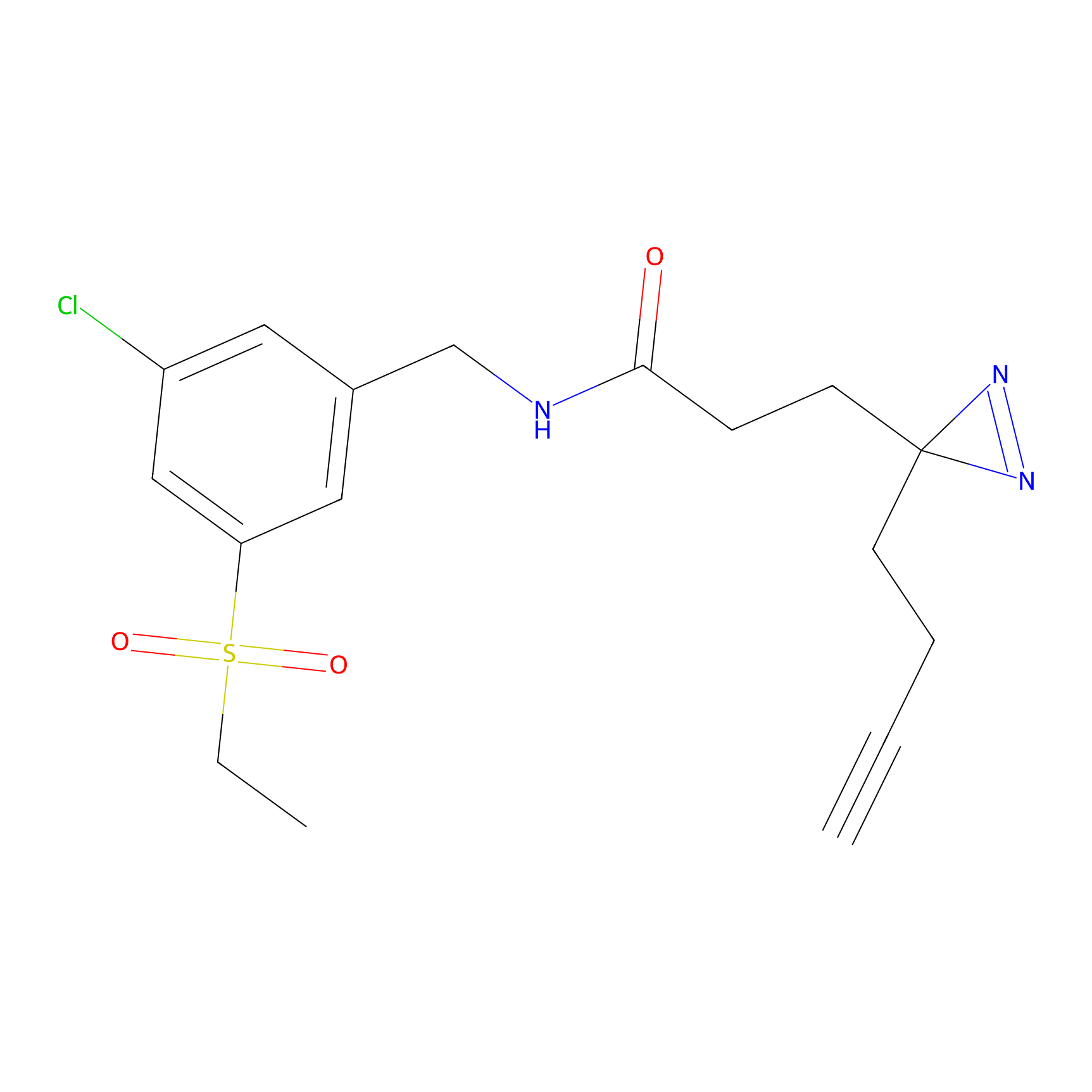
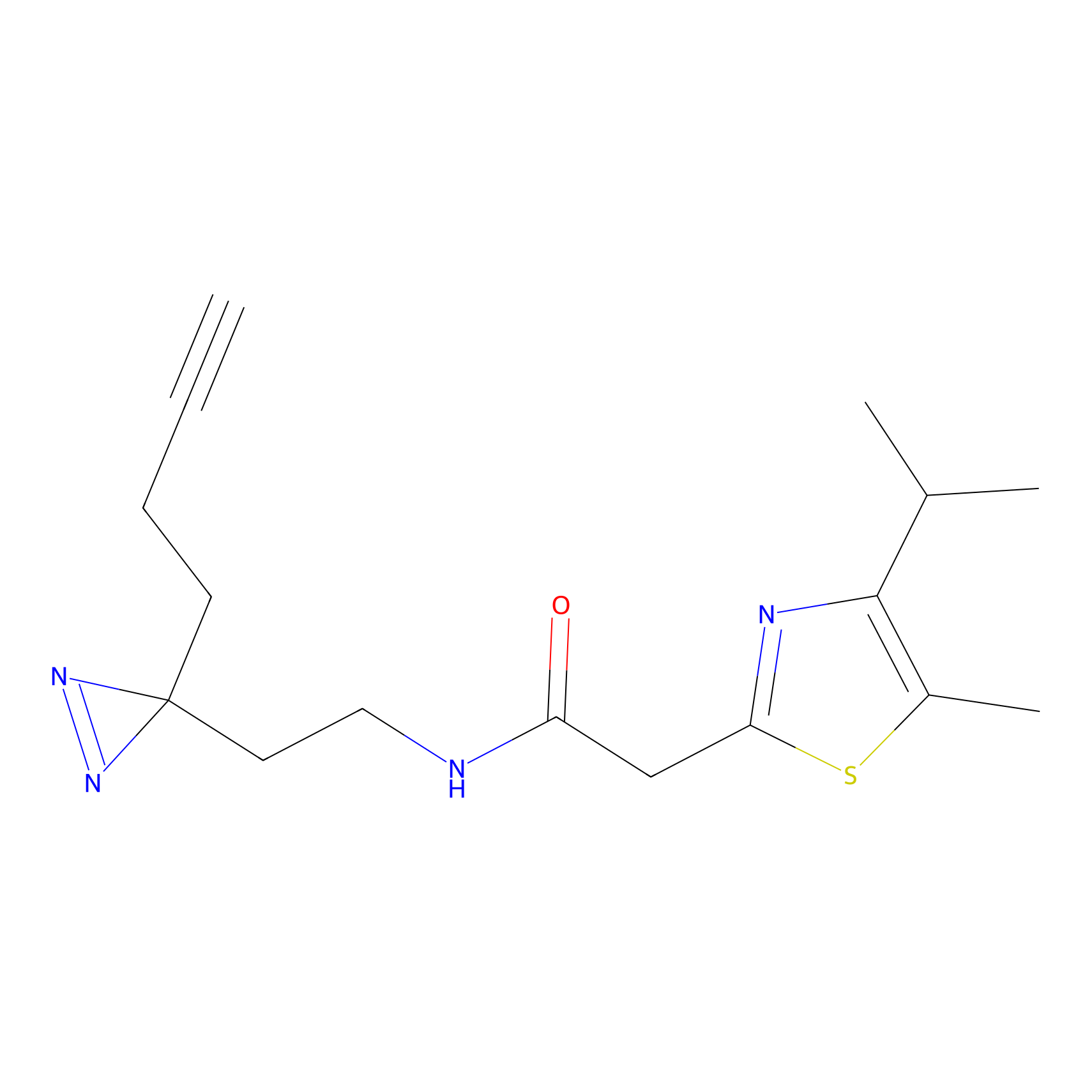
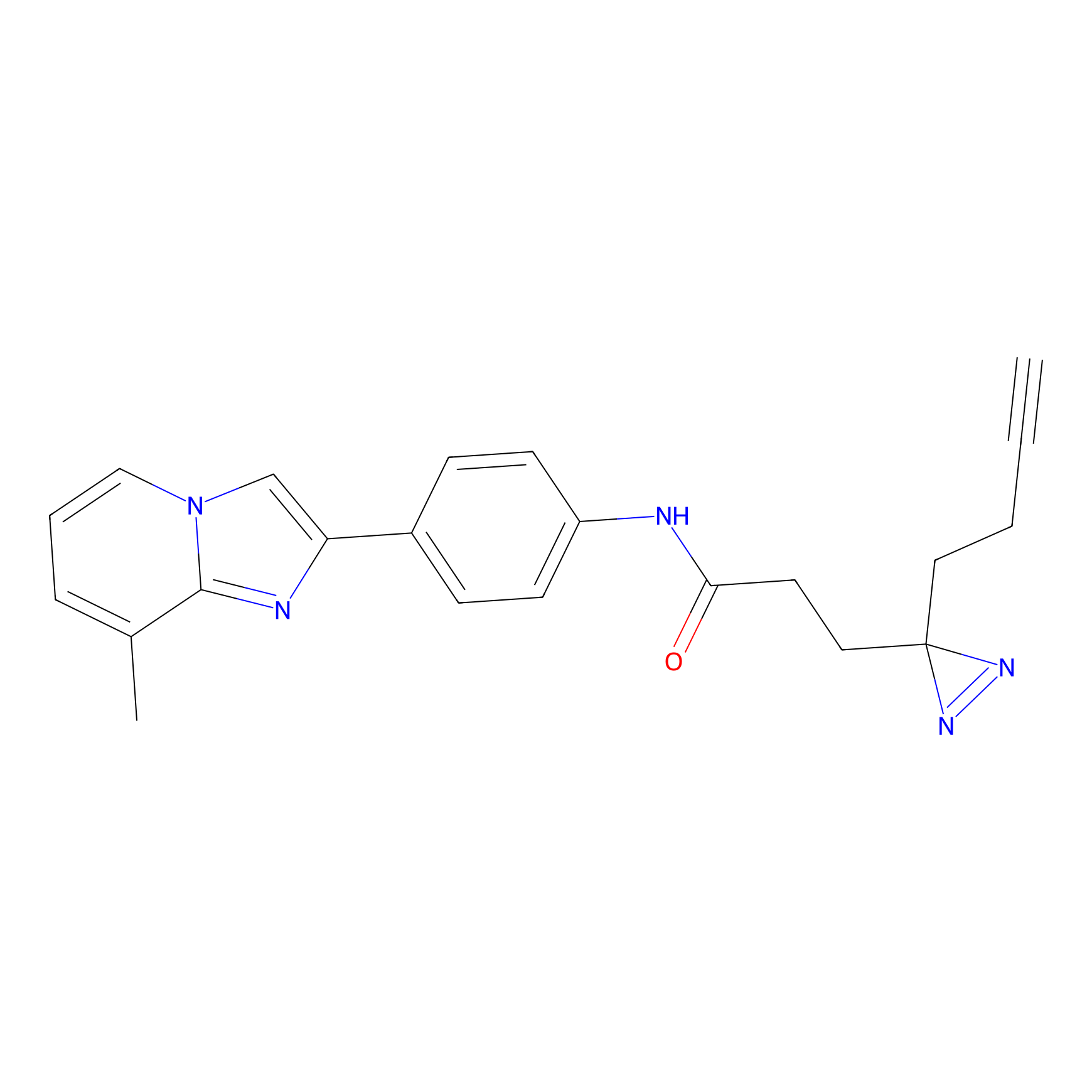
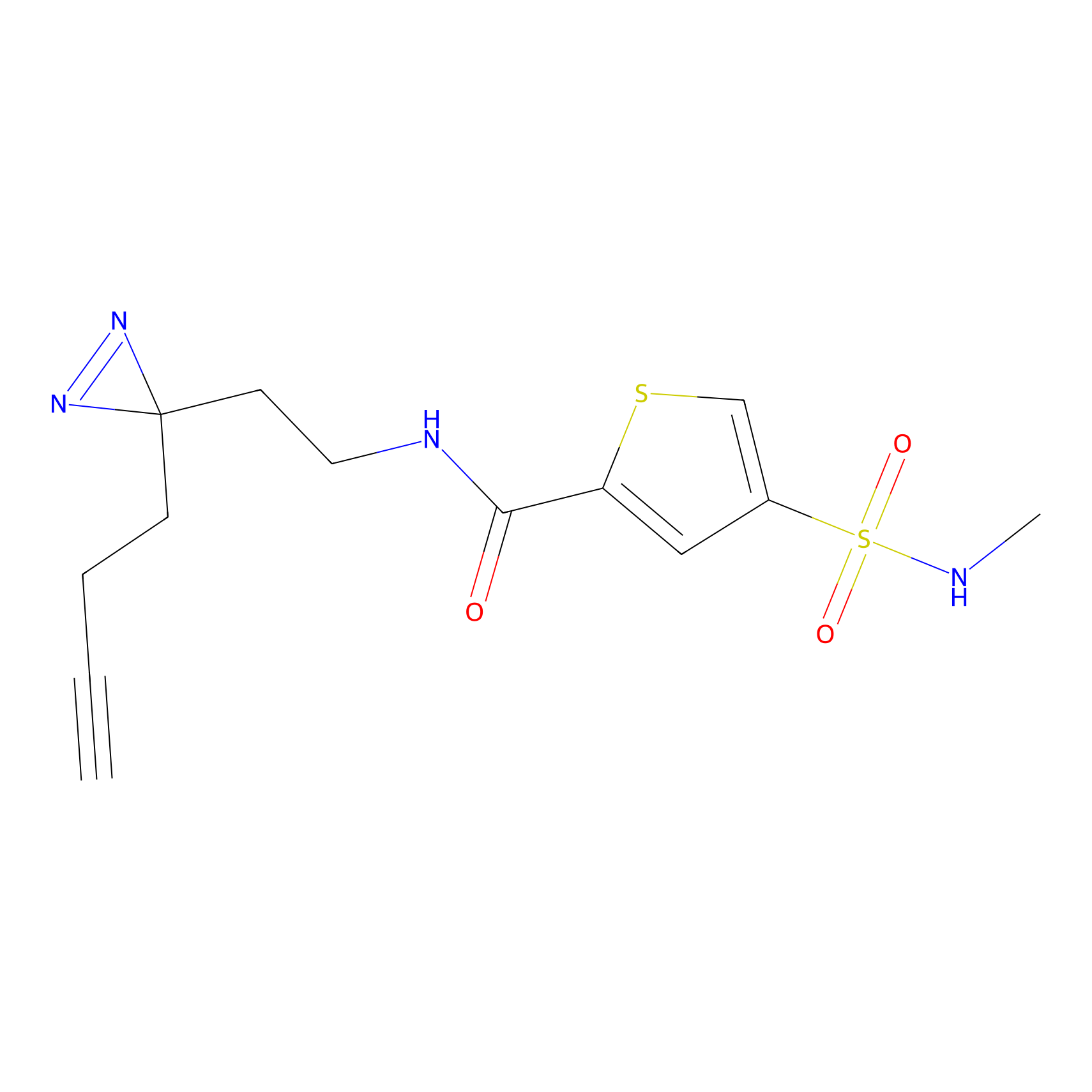
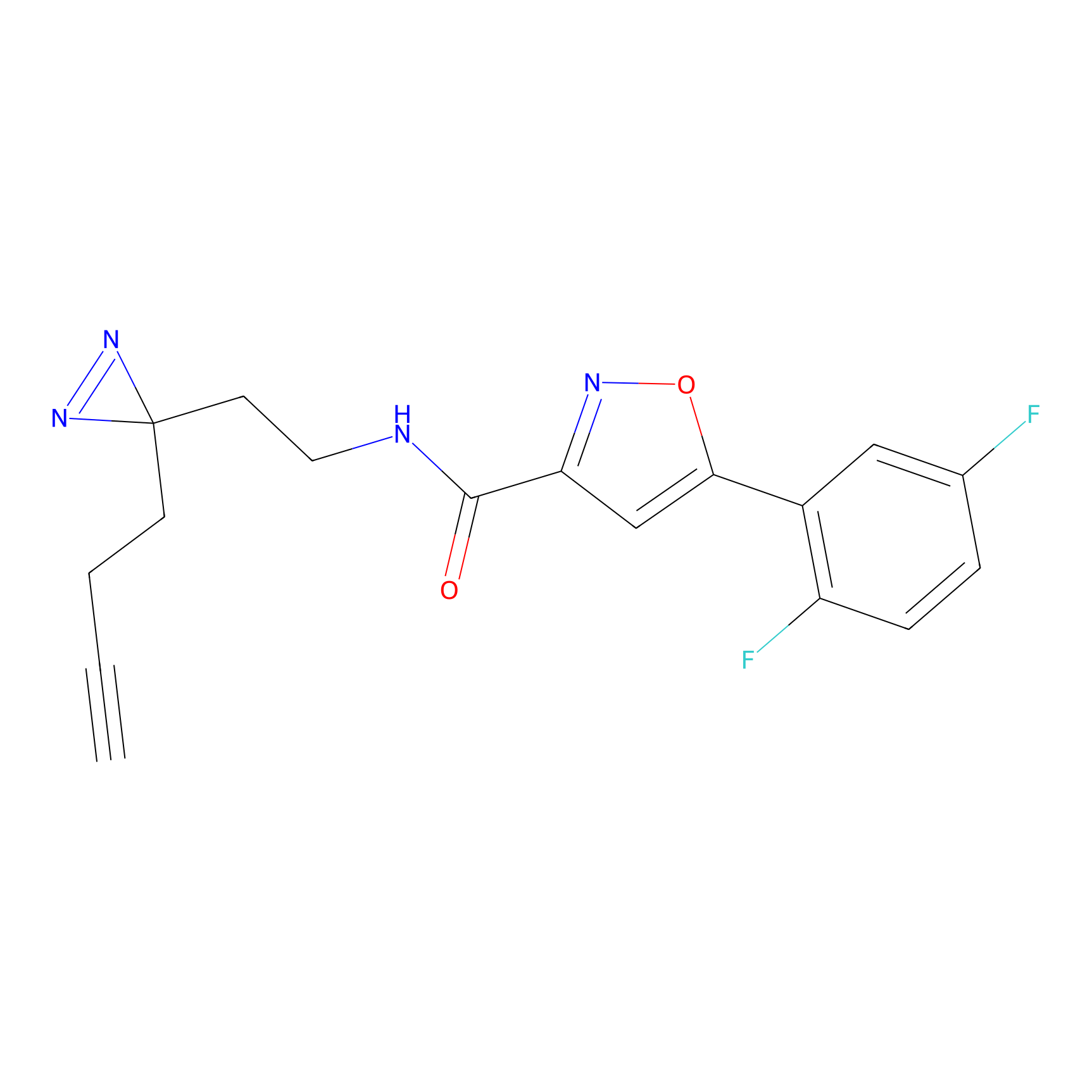
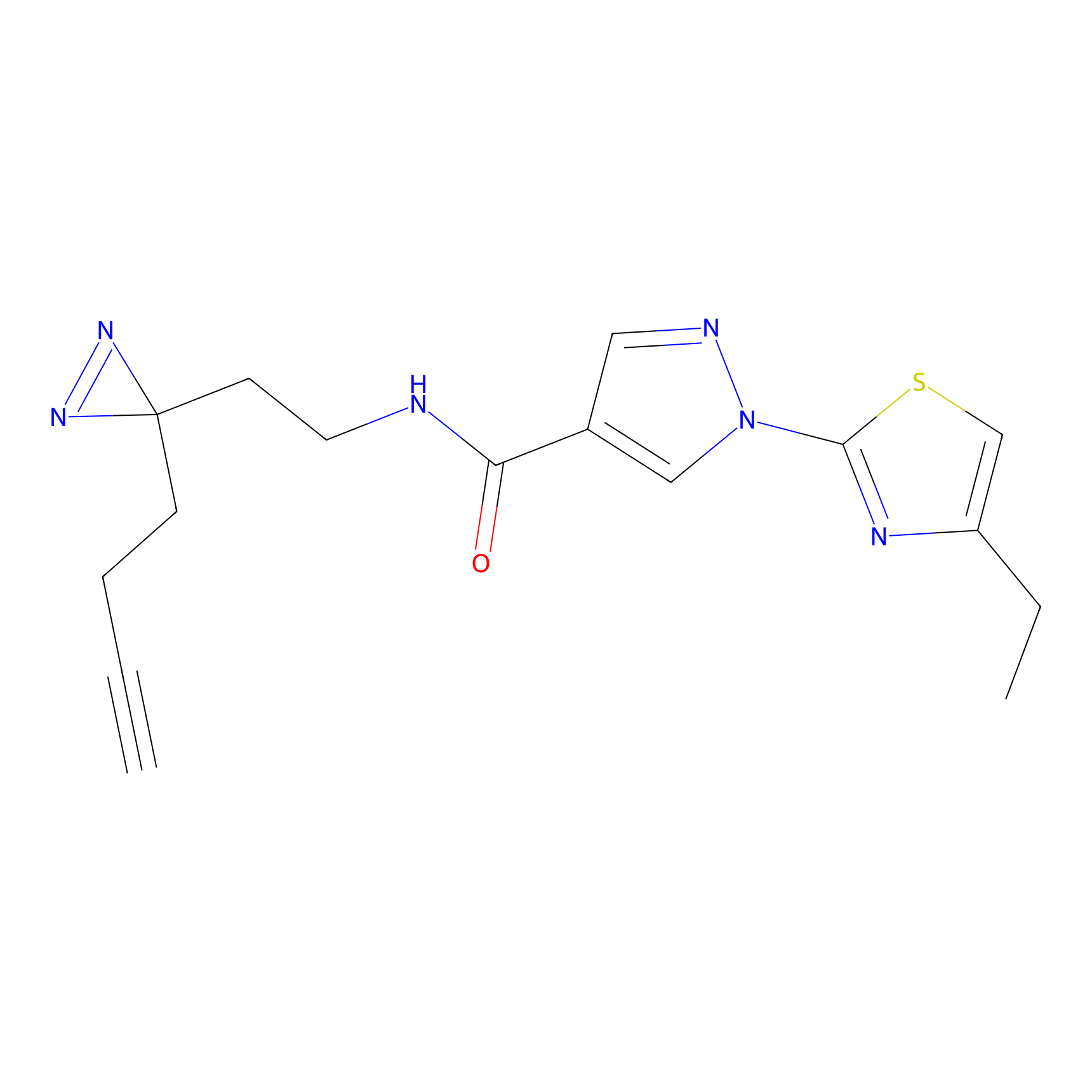
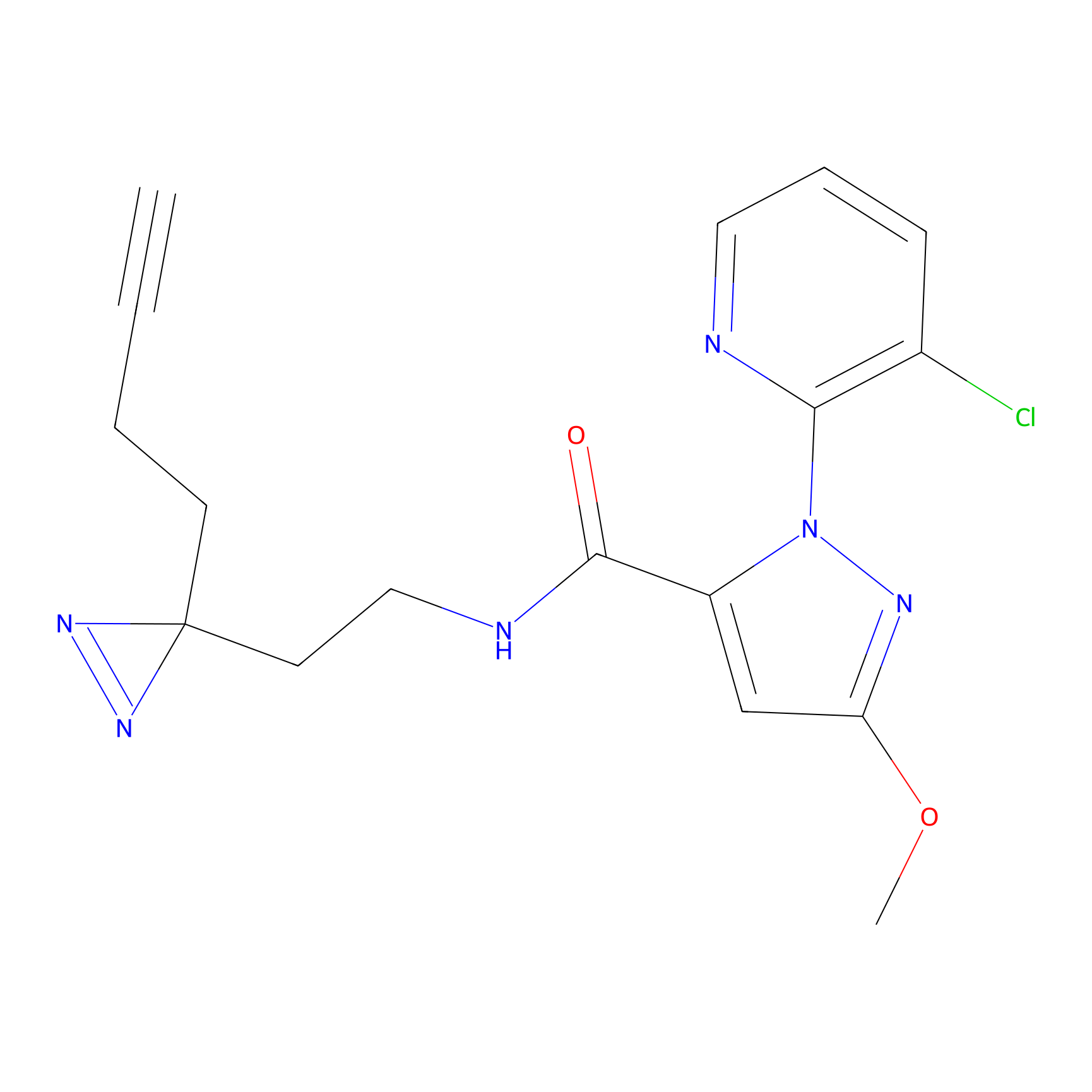
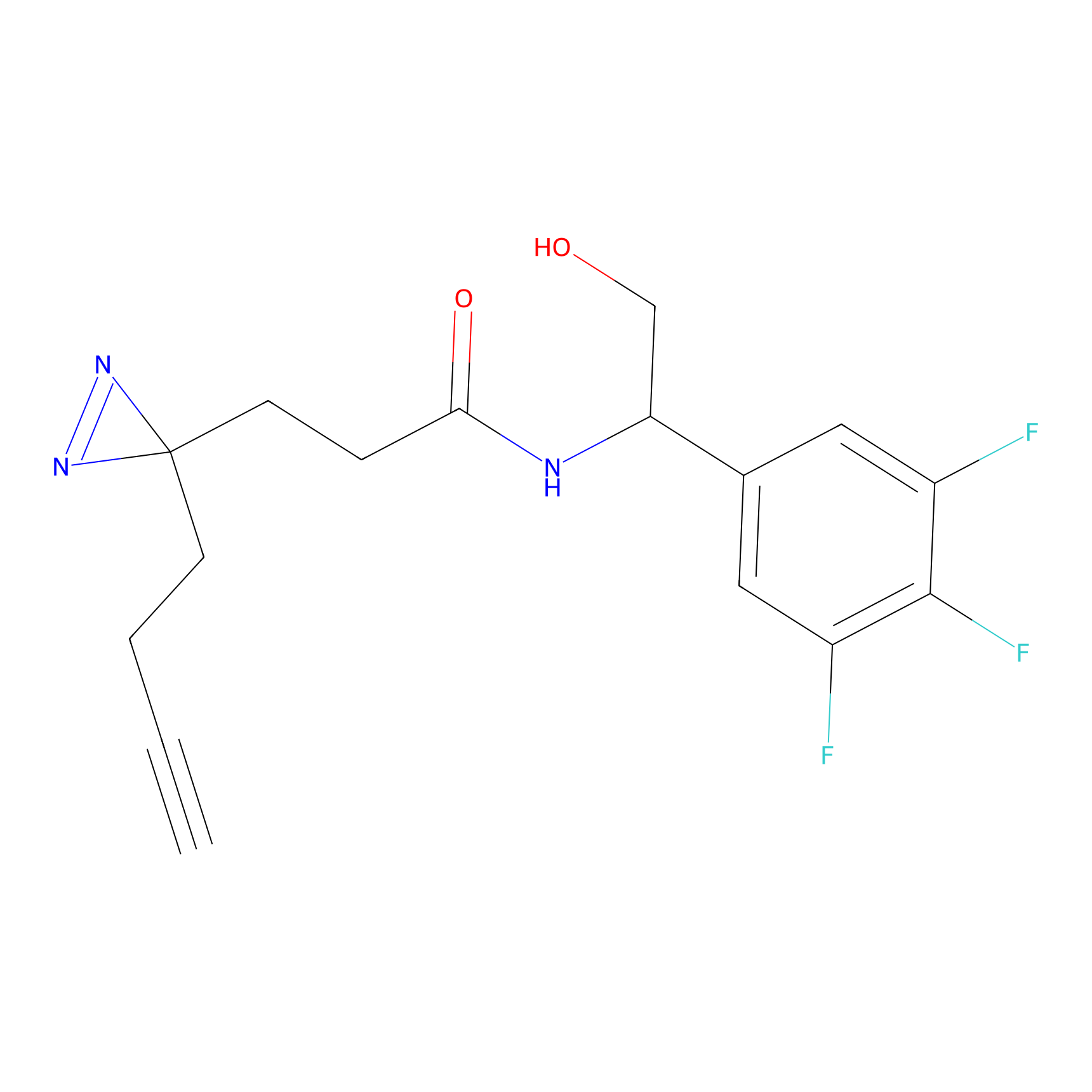
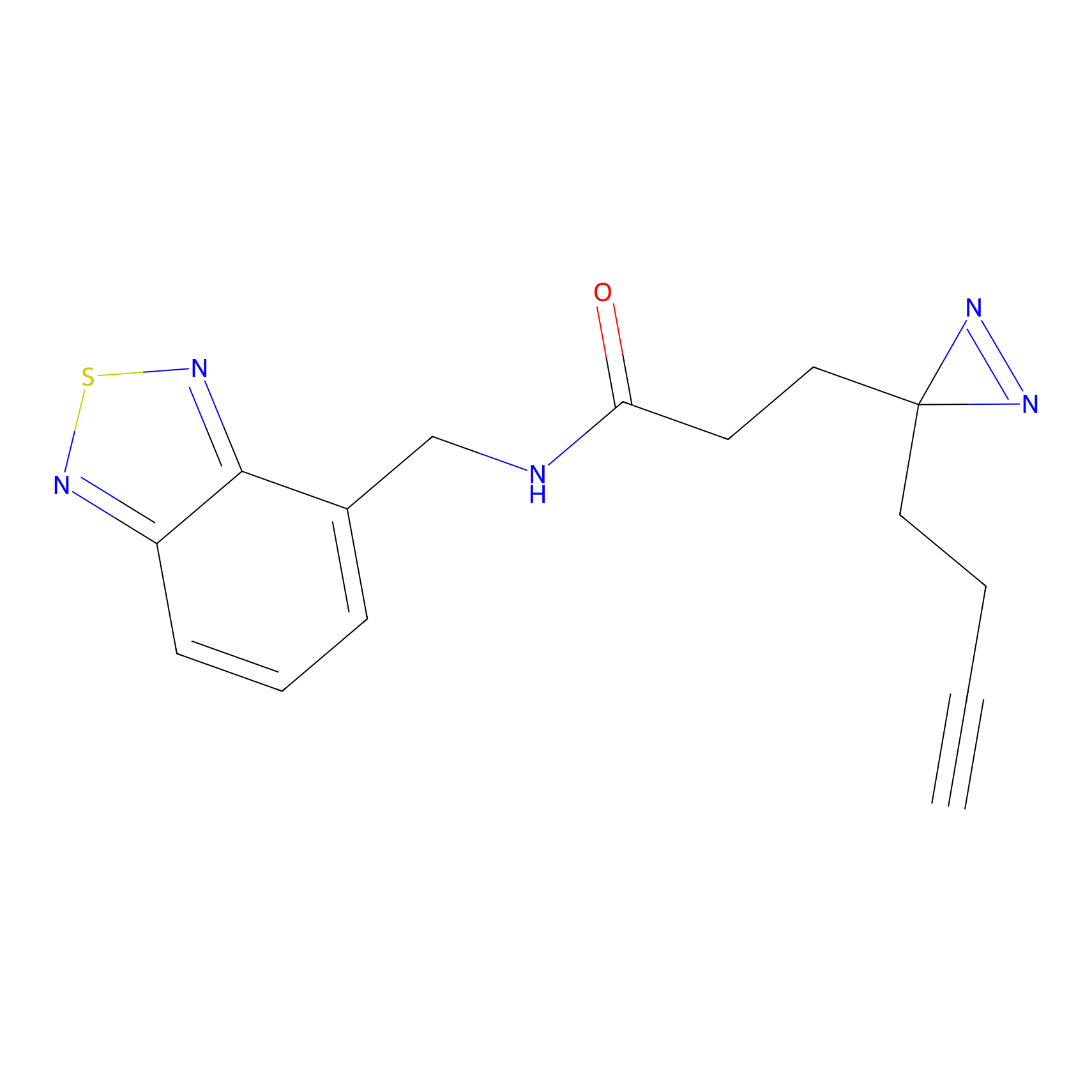
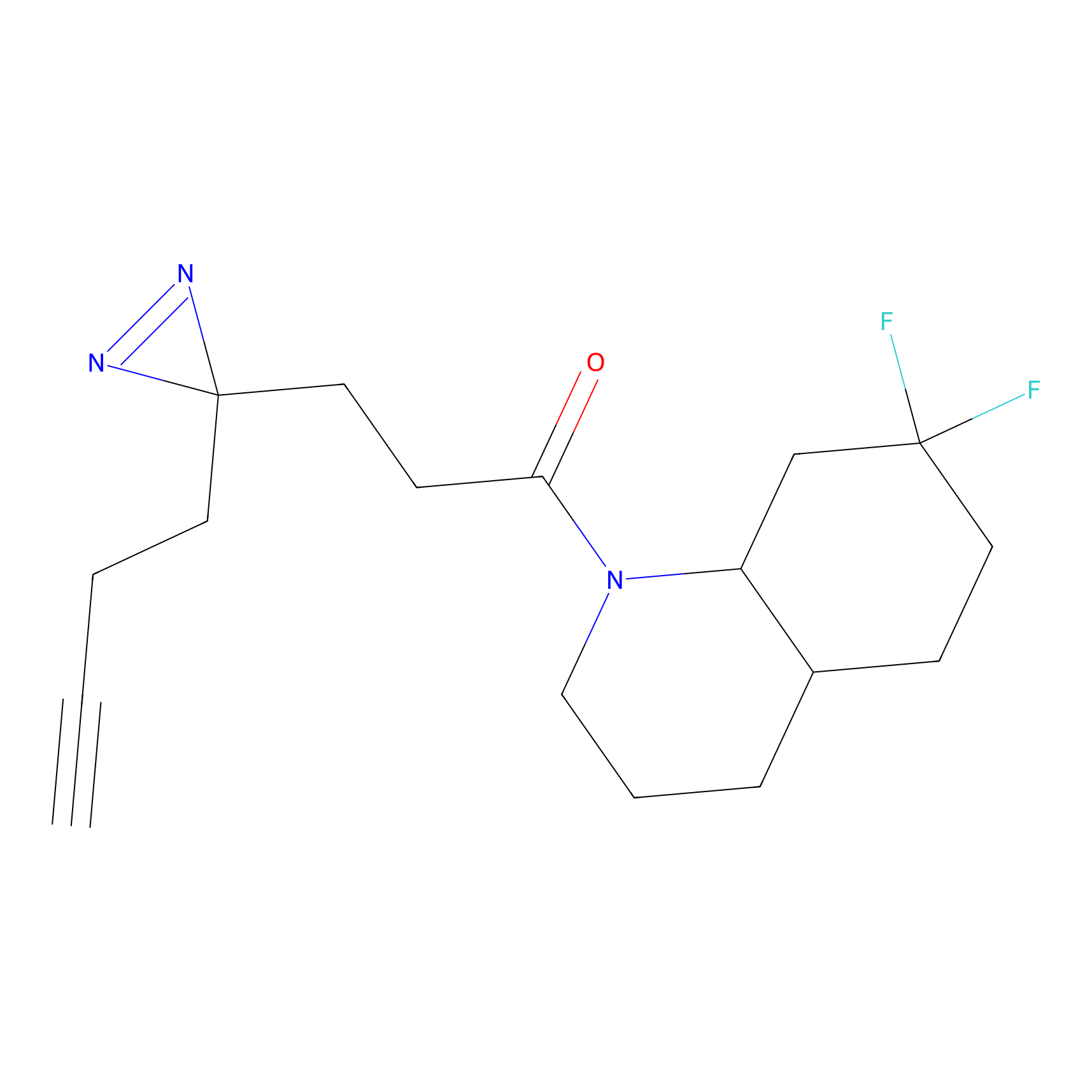
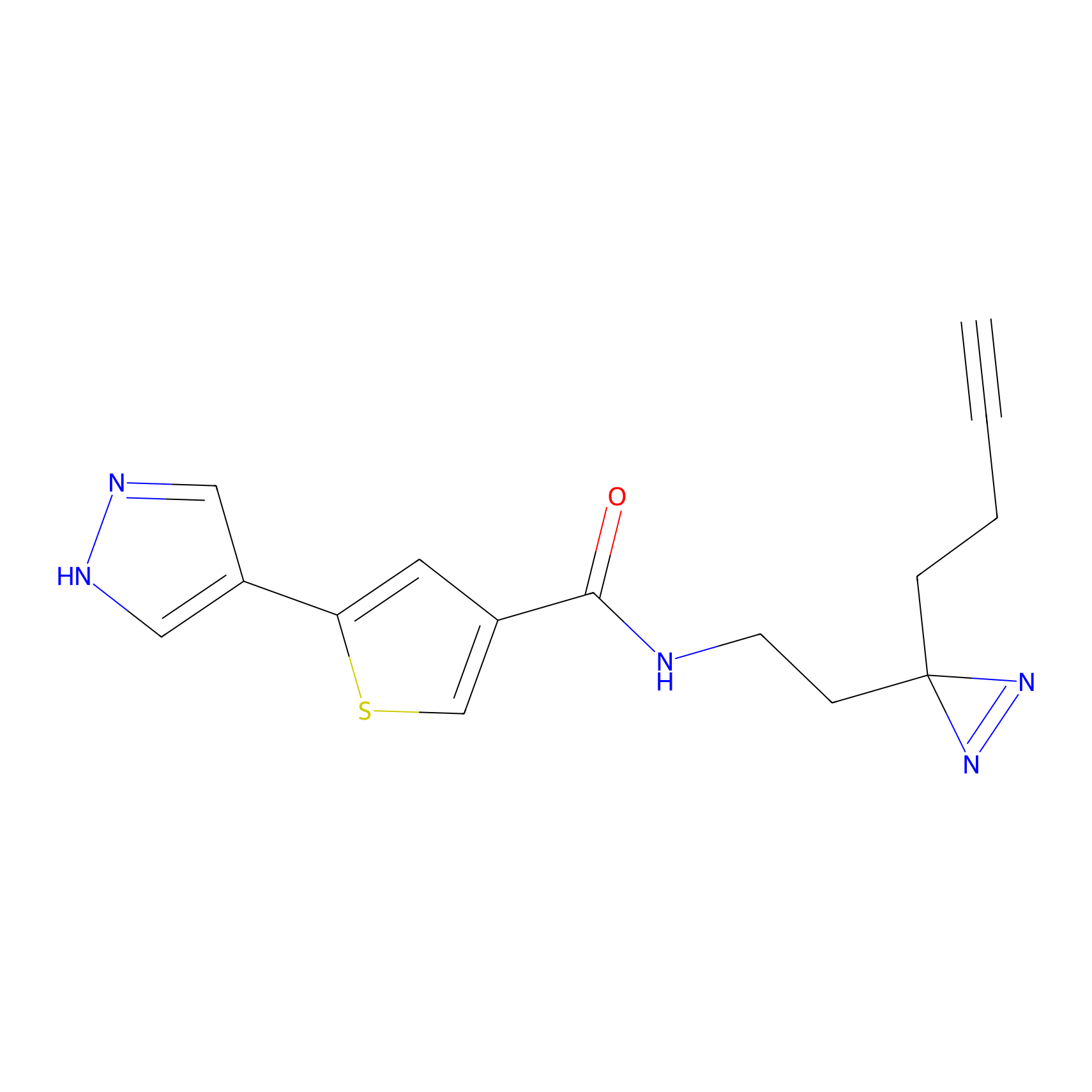
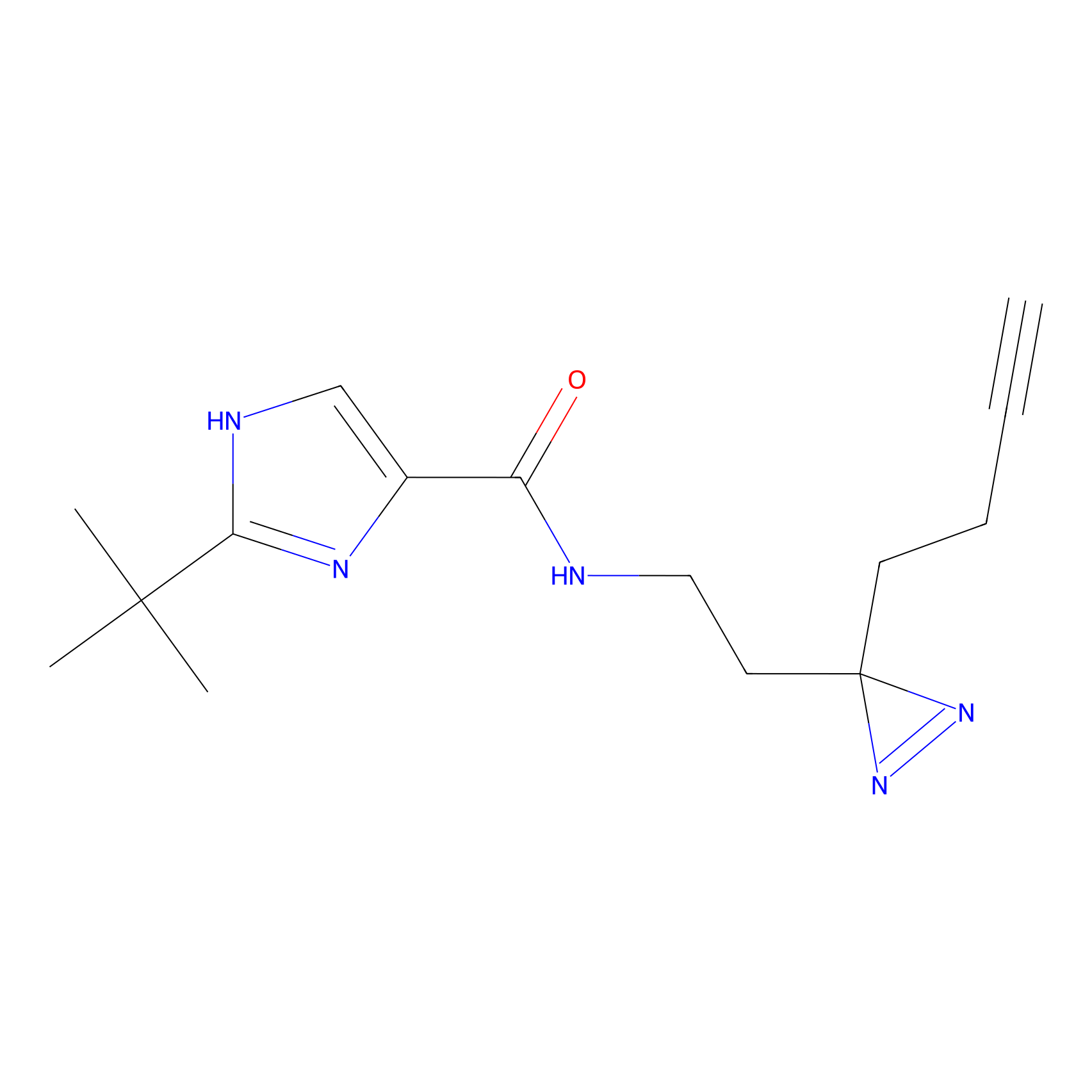
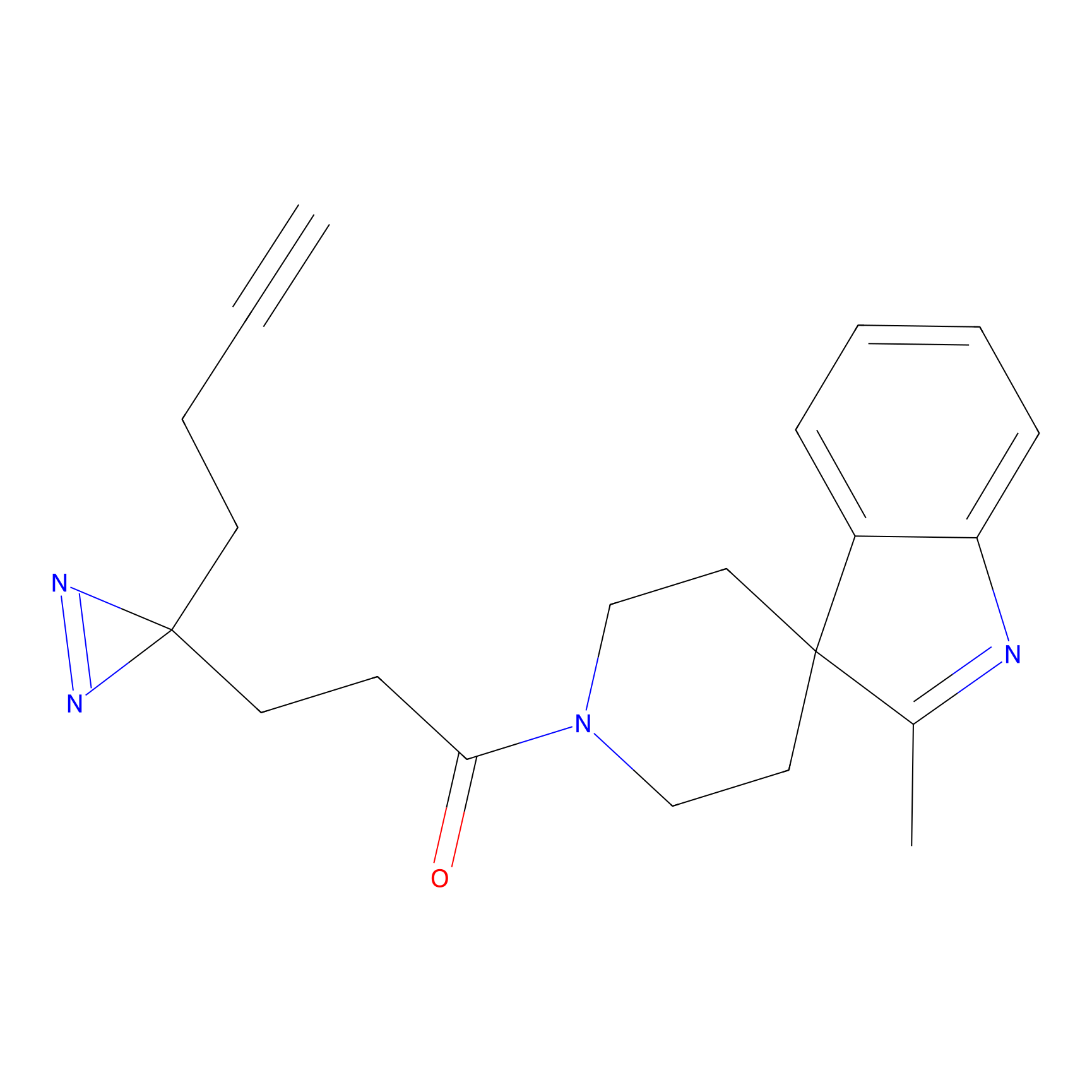
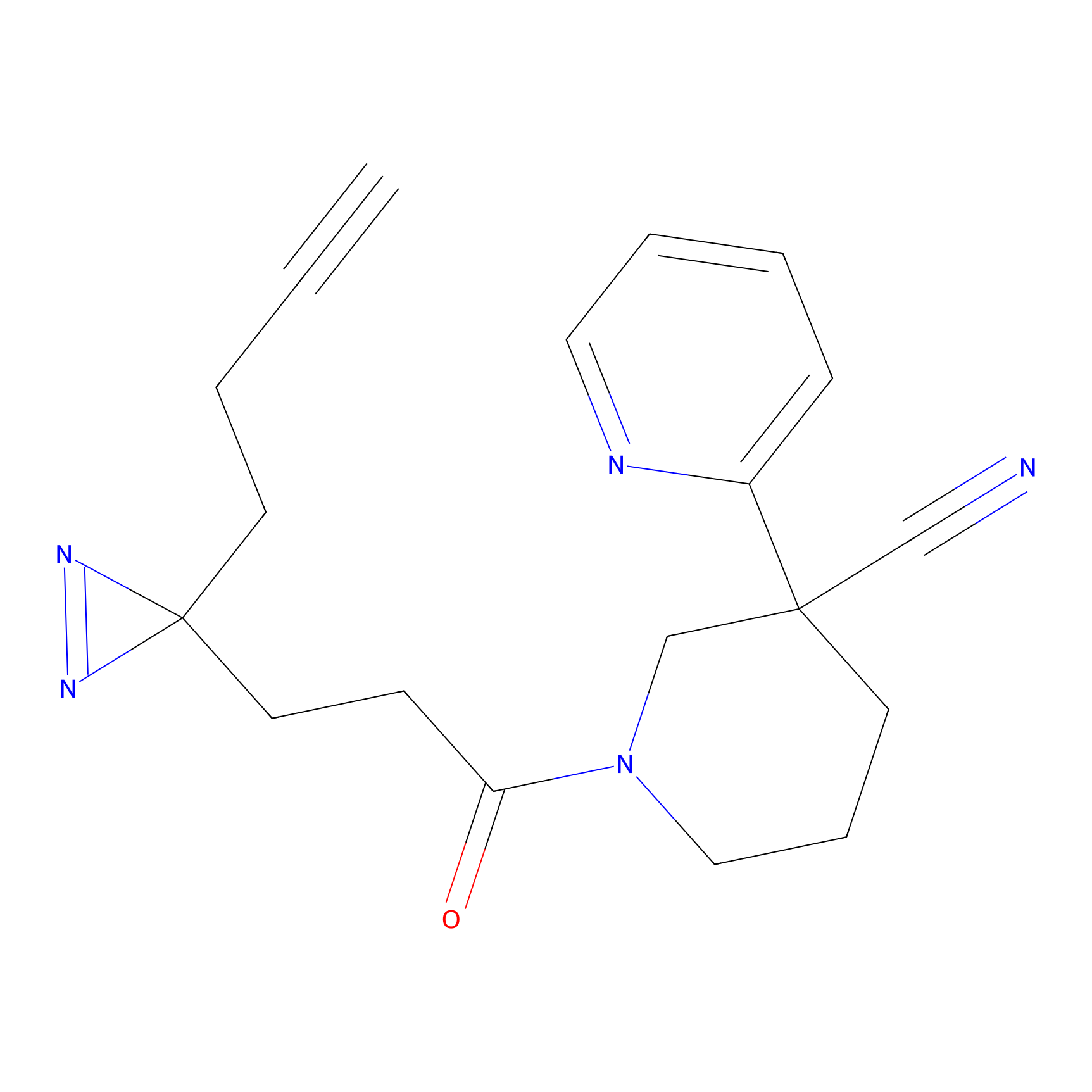
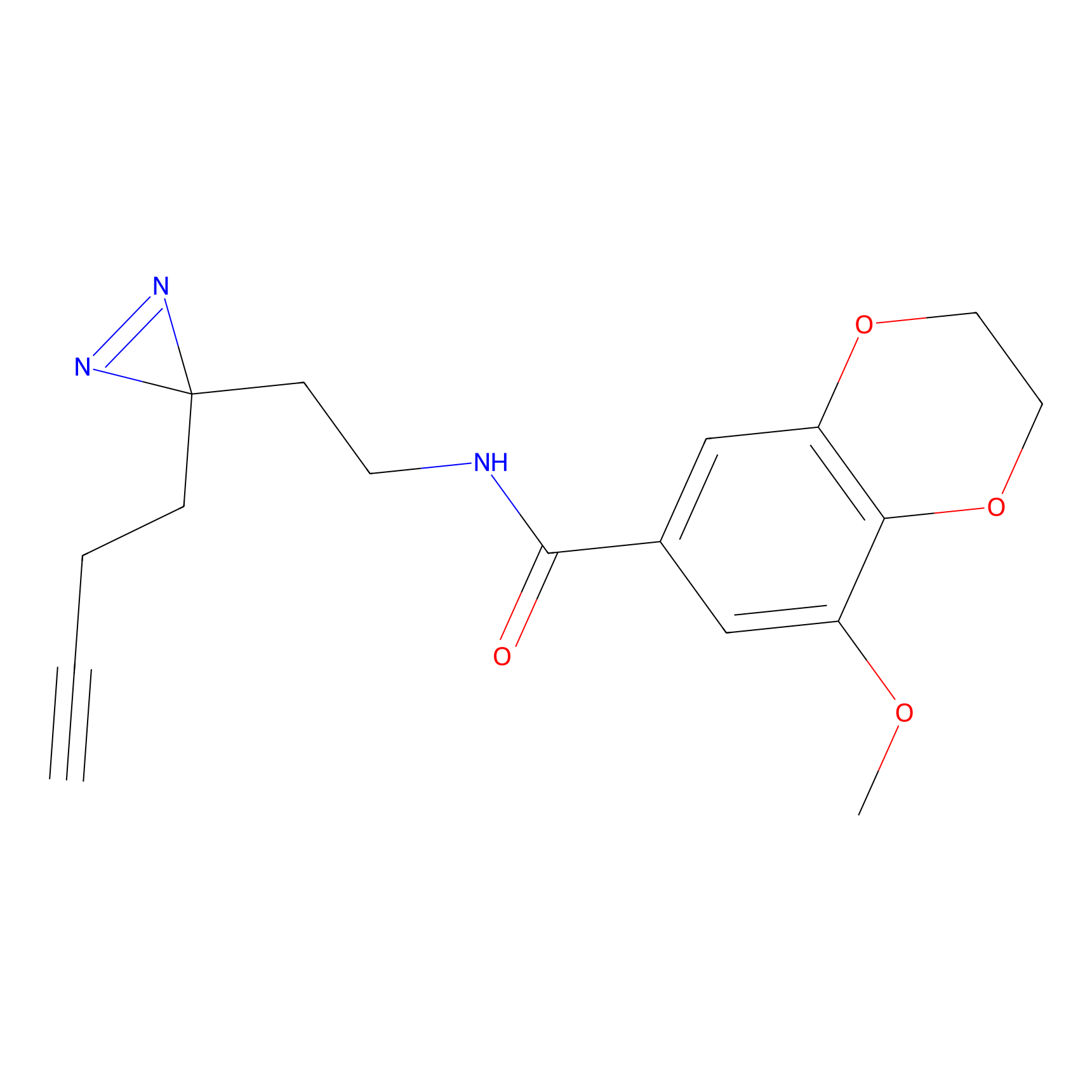
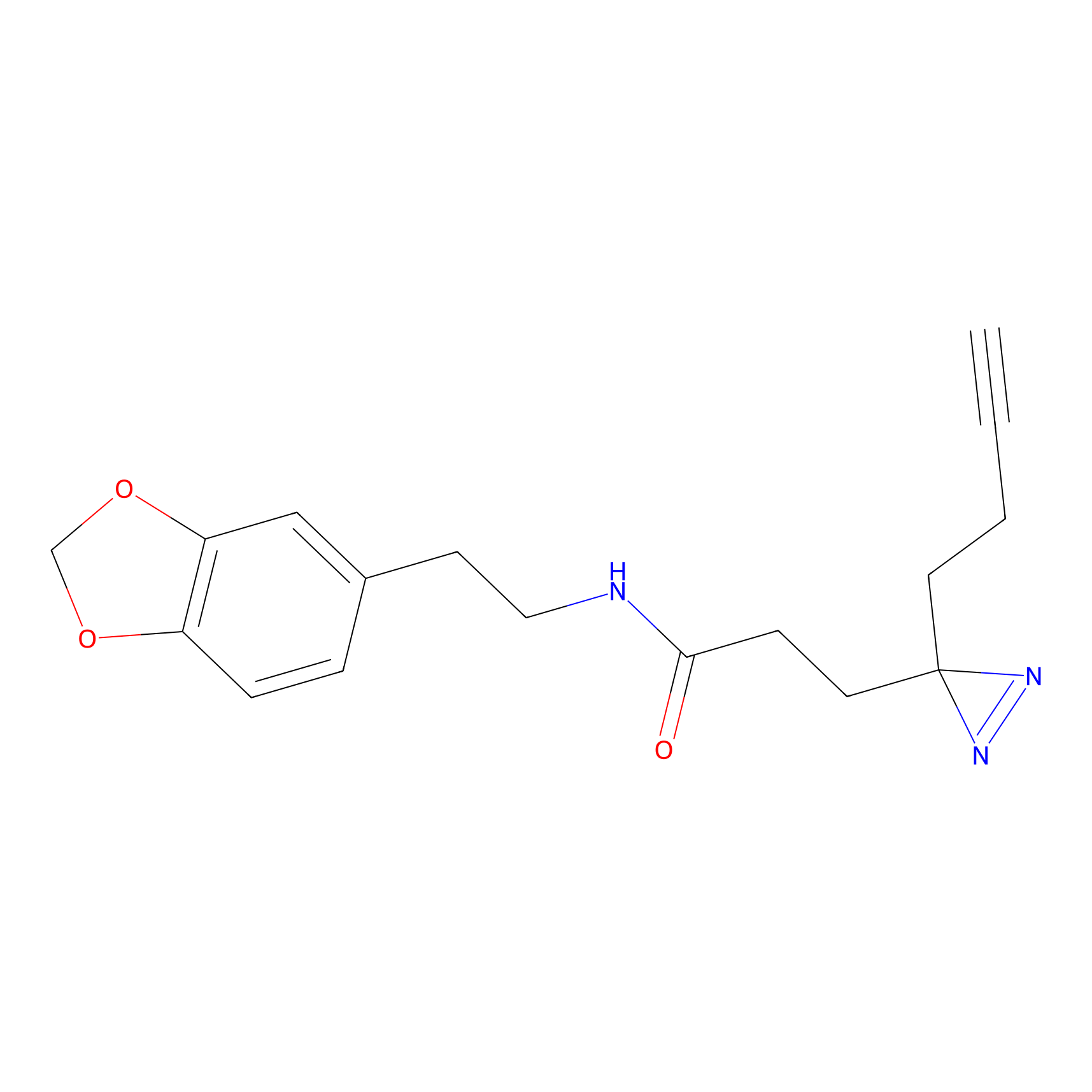
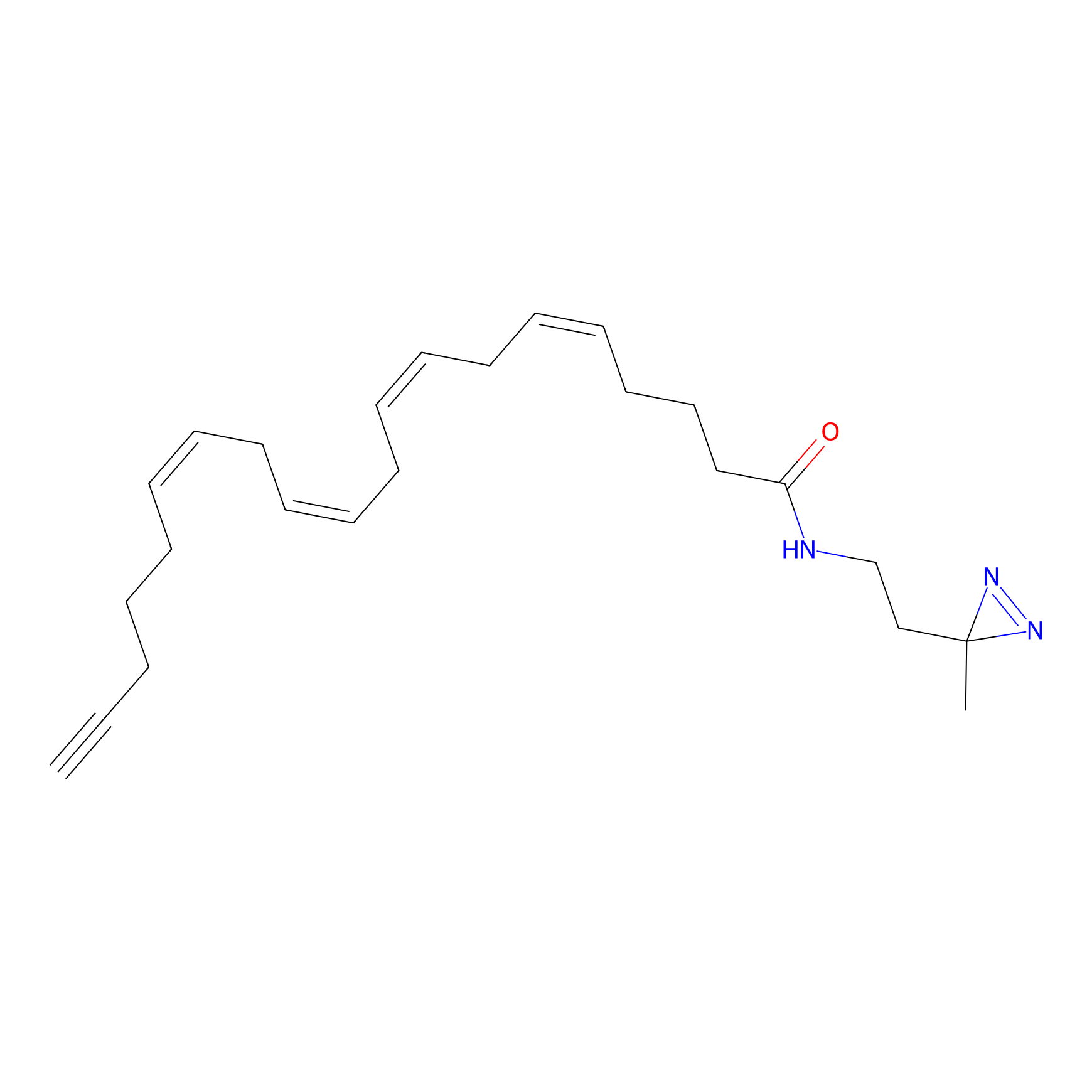
AZ-9 Probe Info |
 |
3.95 | LDD0393 | [1] | |
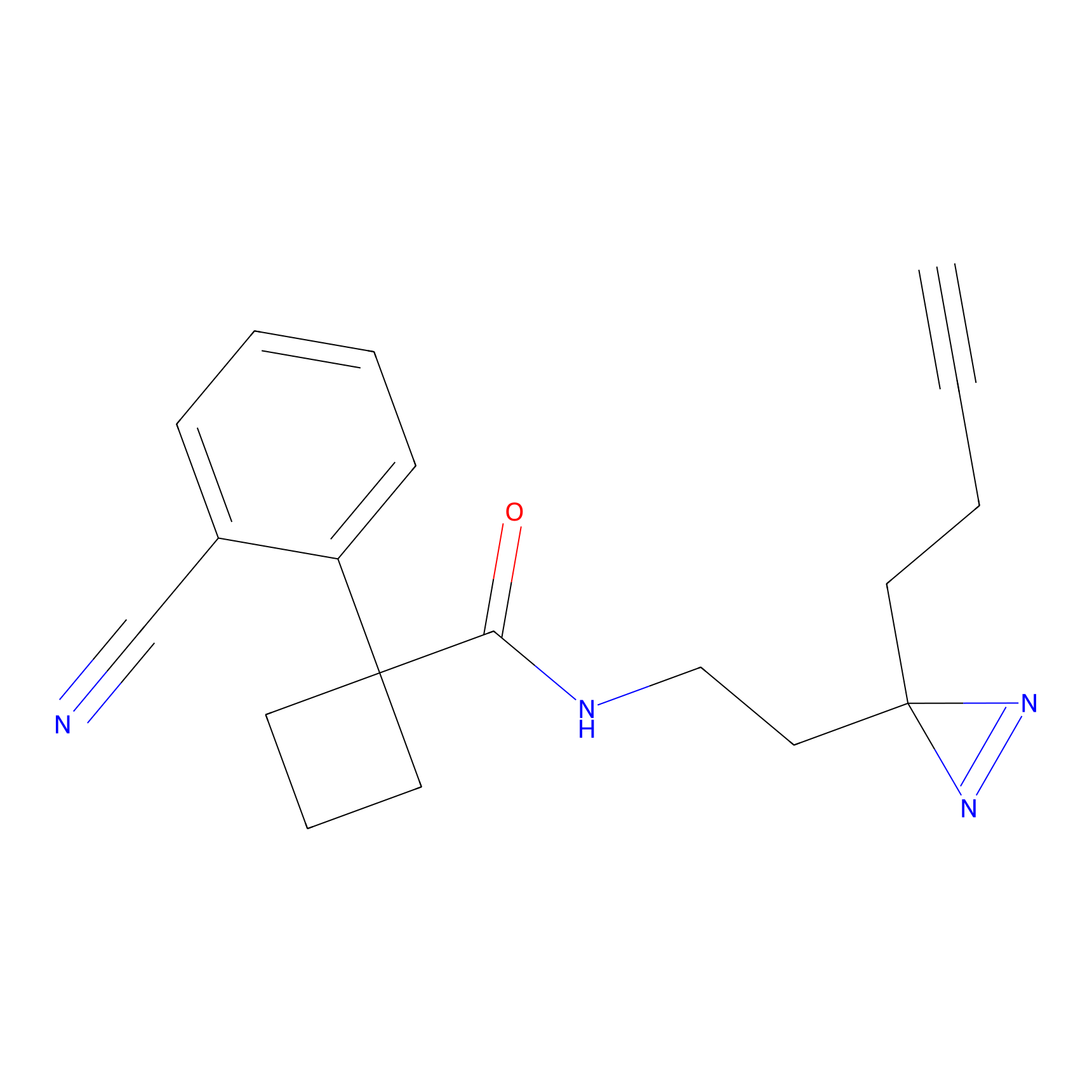
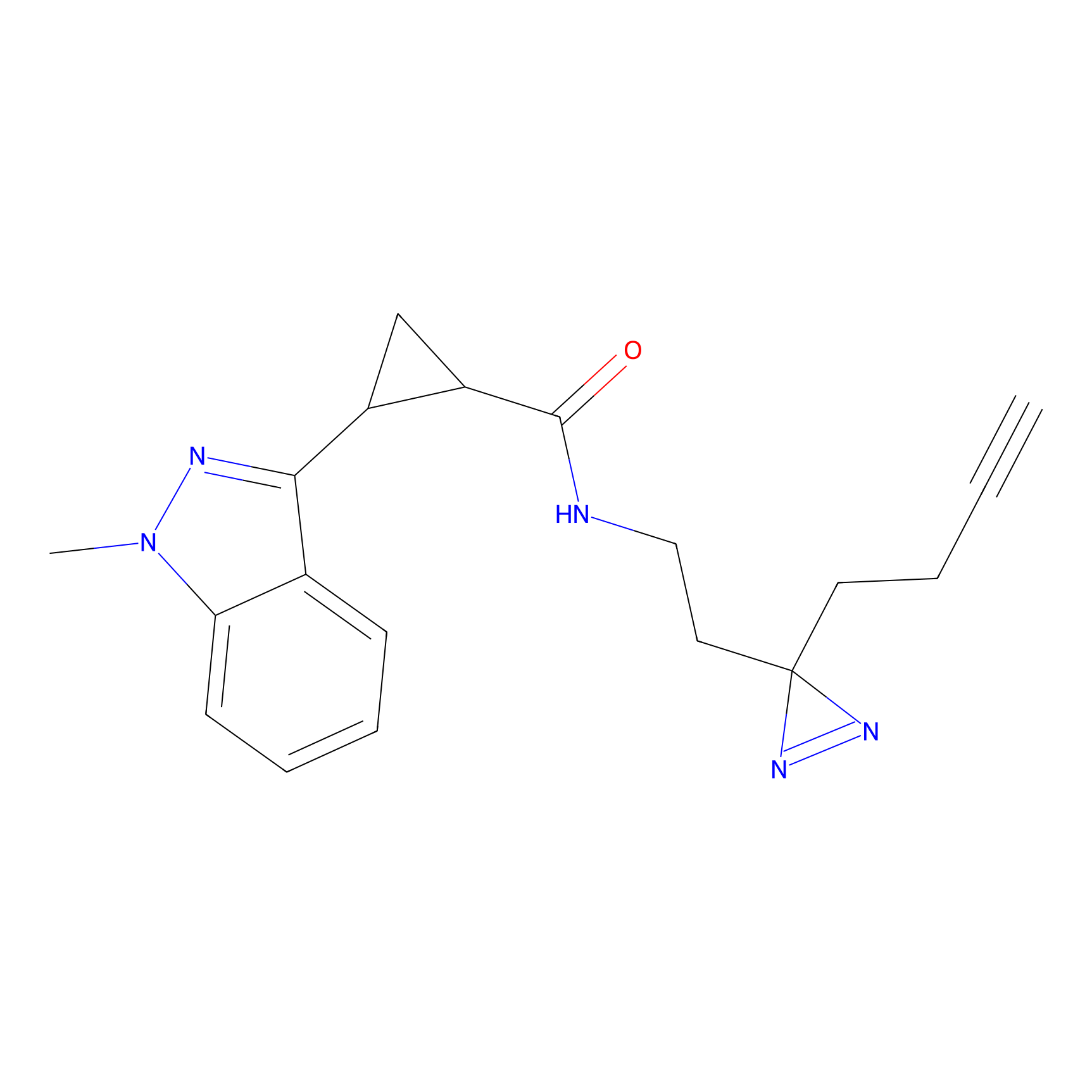
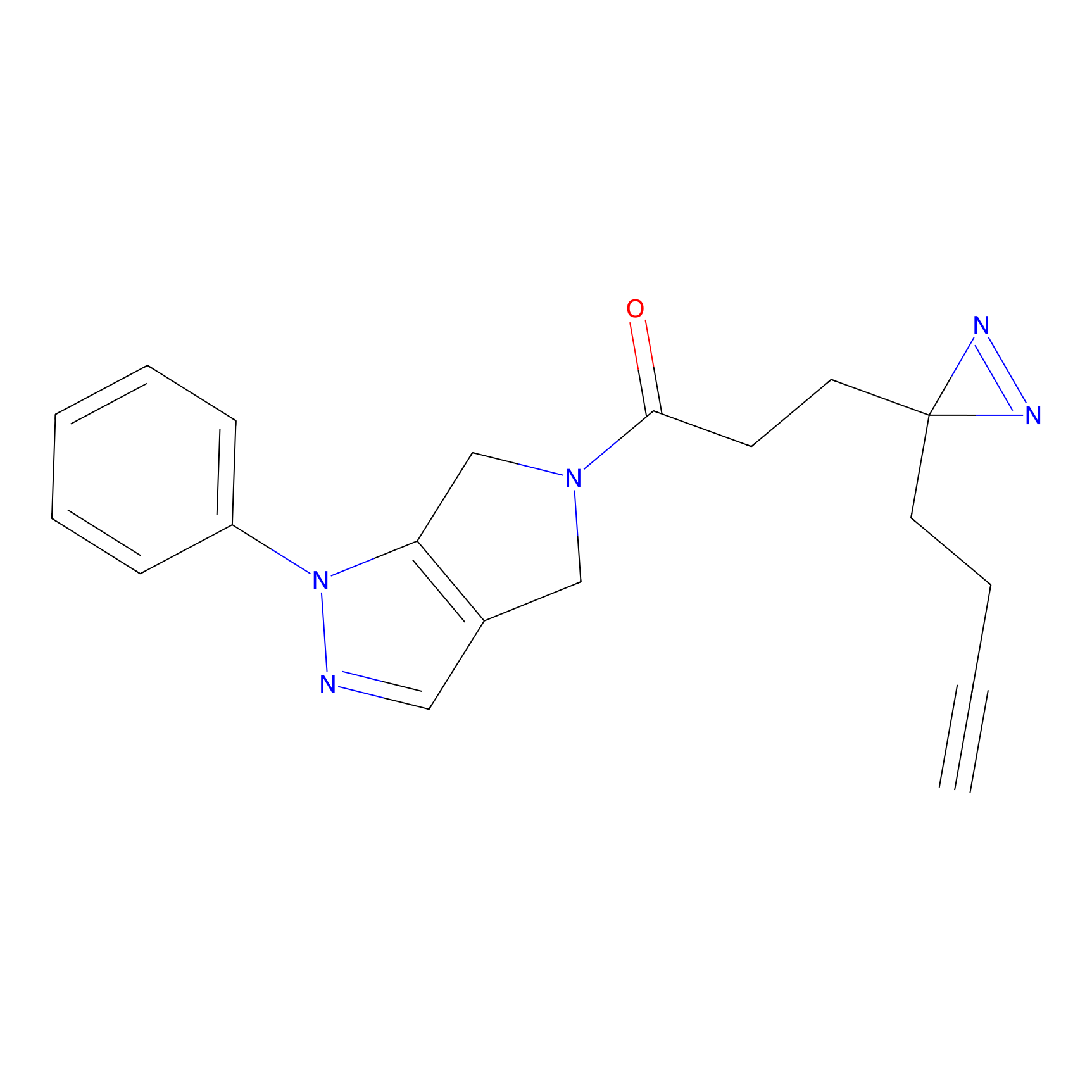
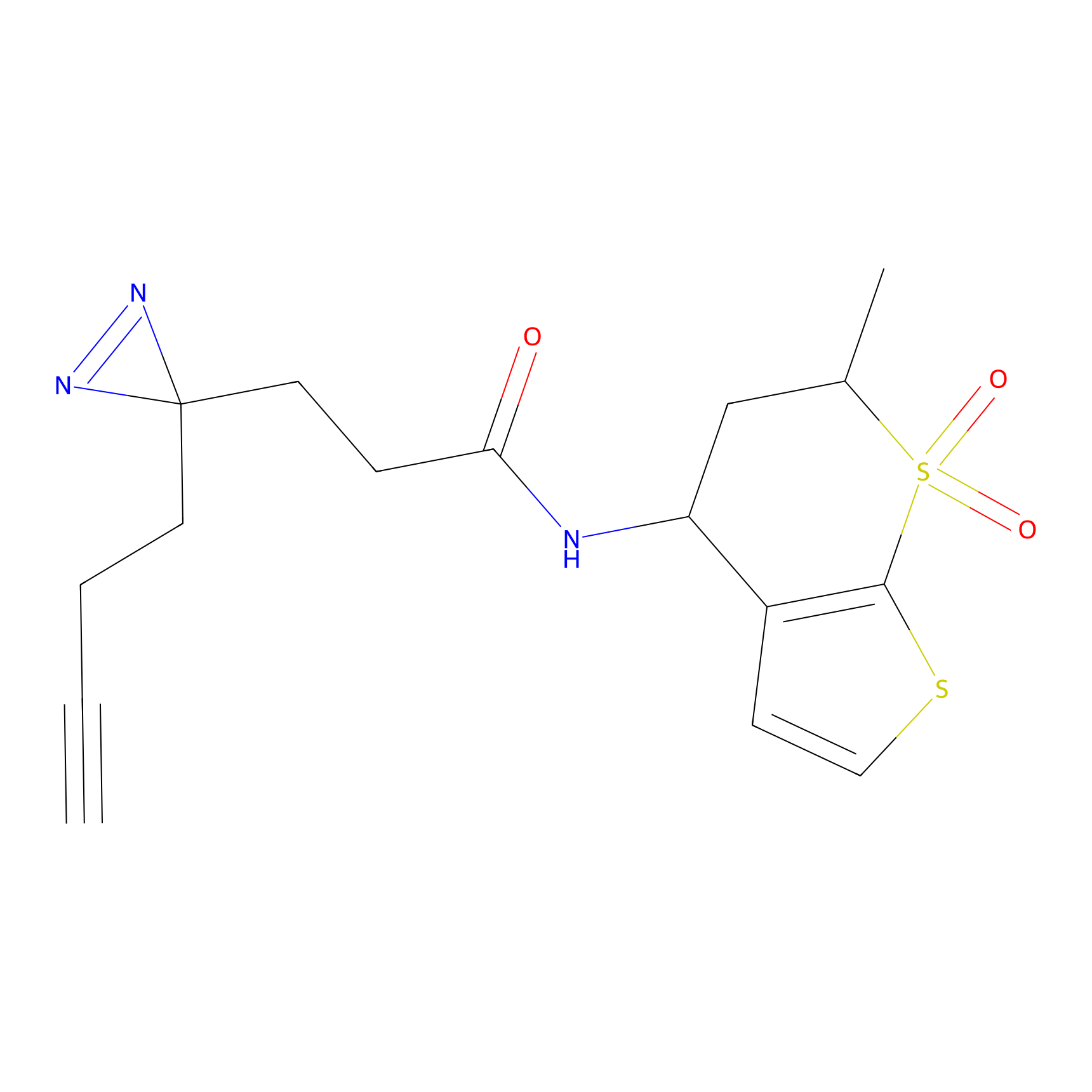
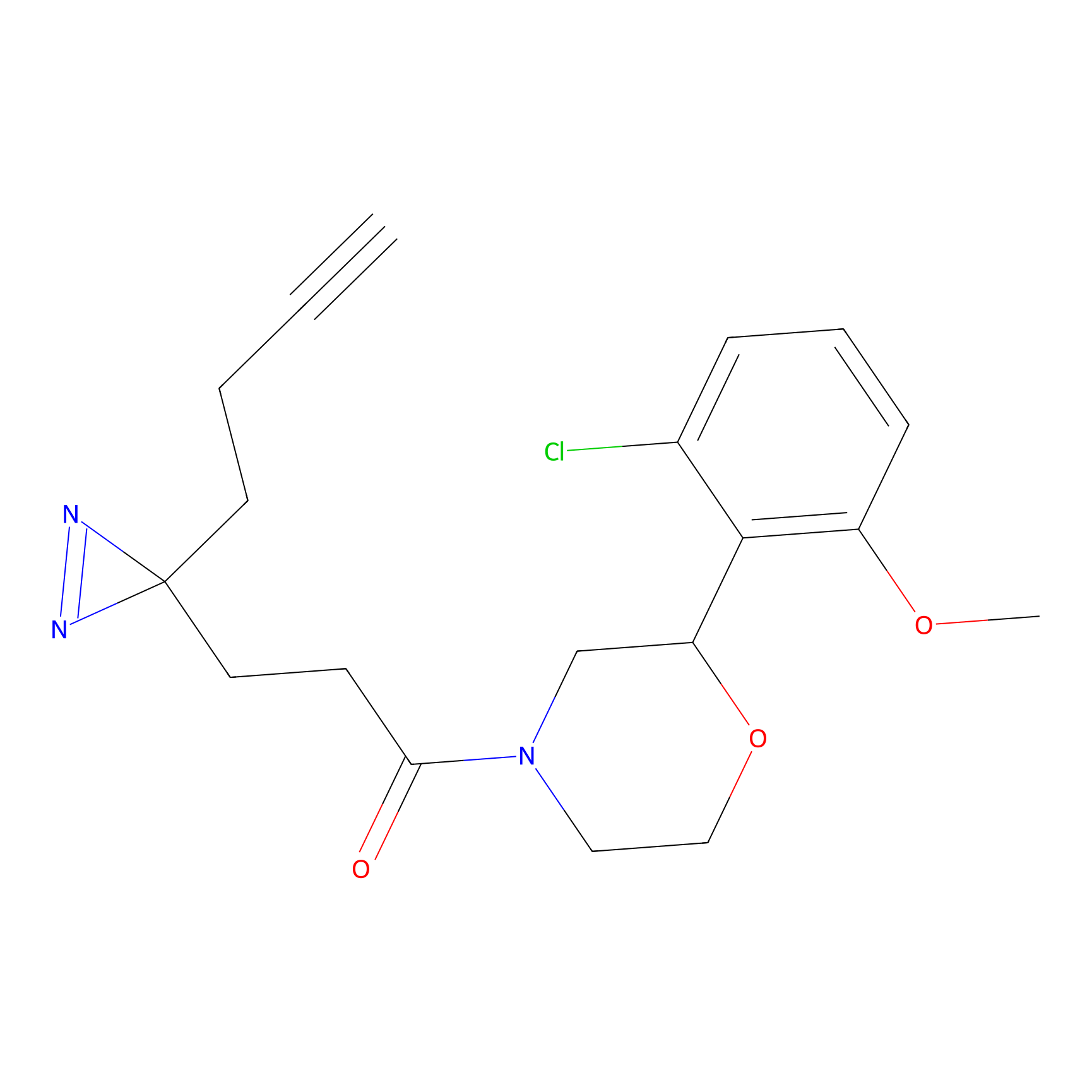
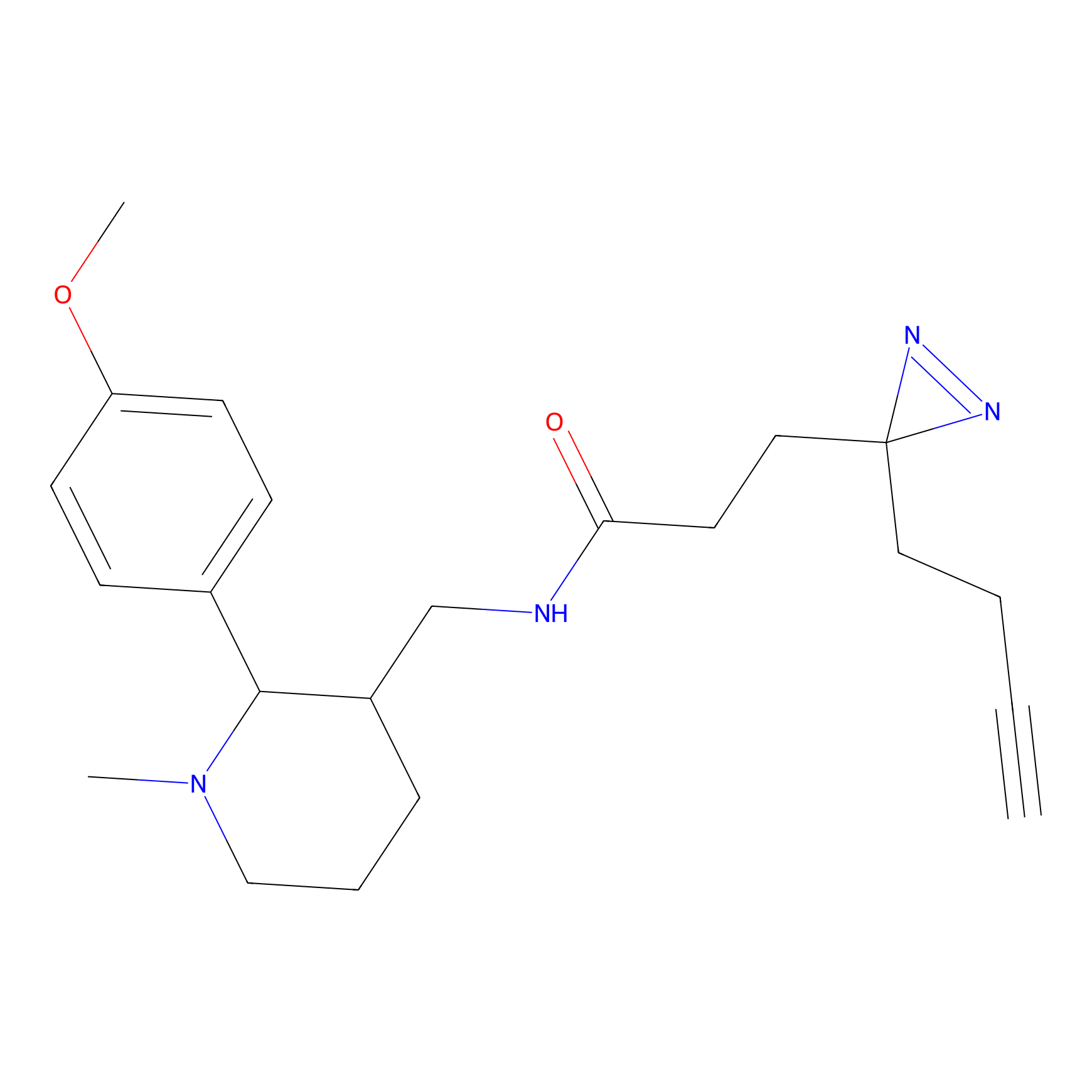
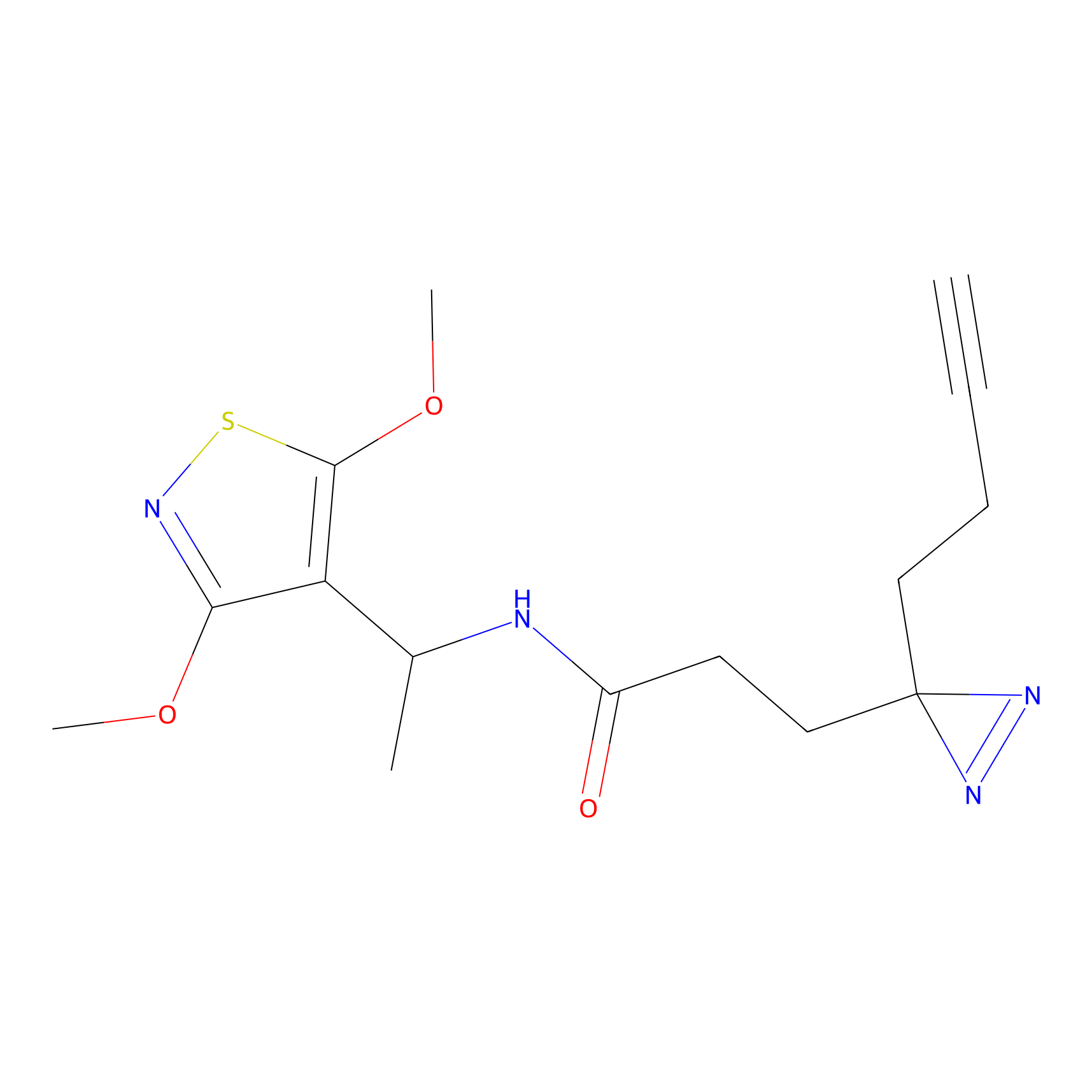
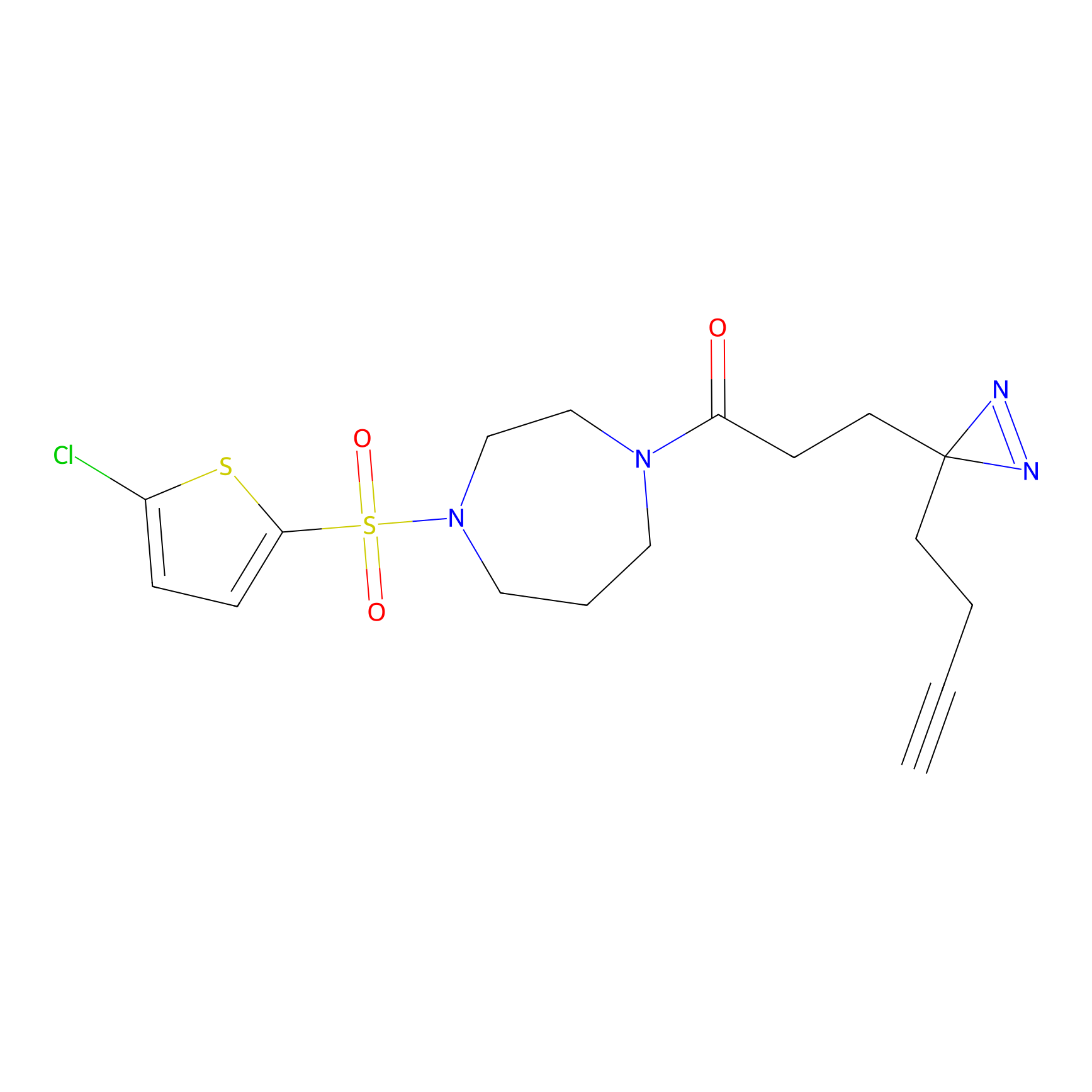
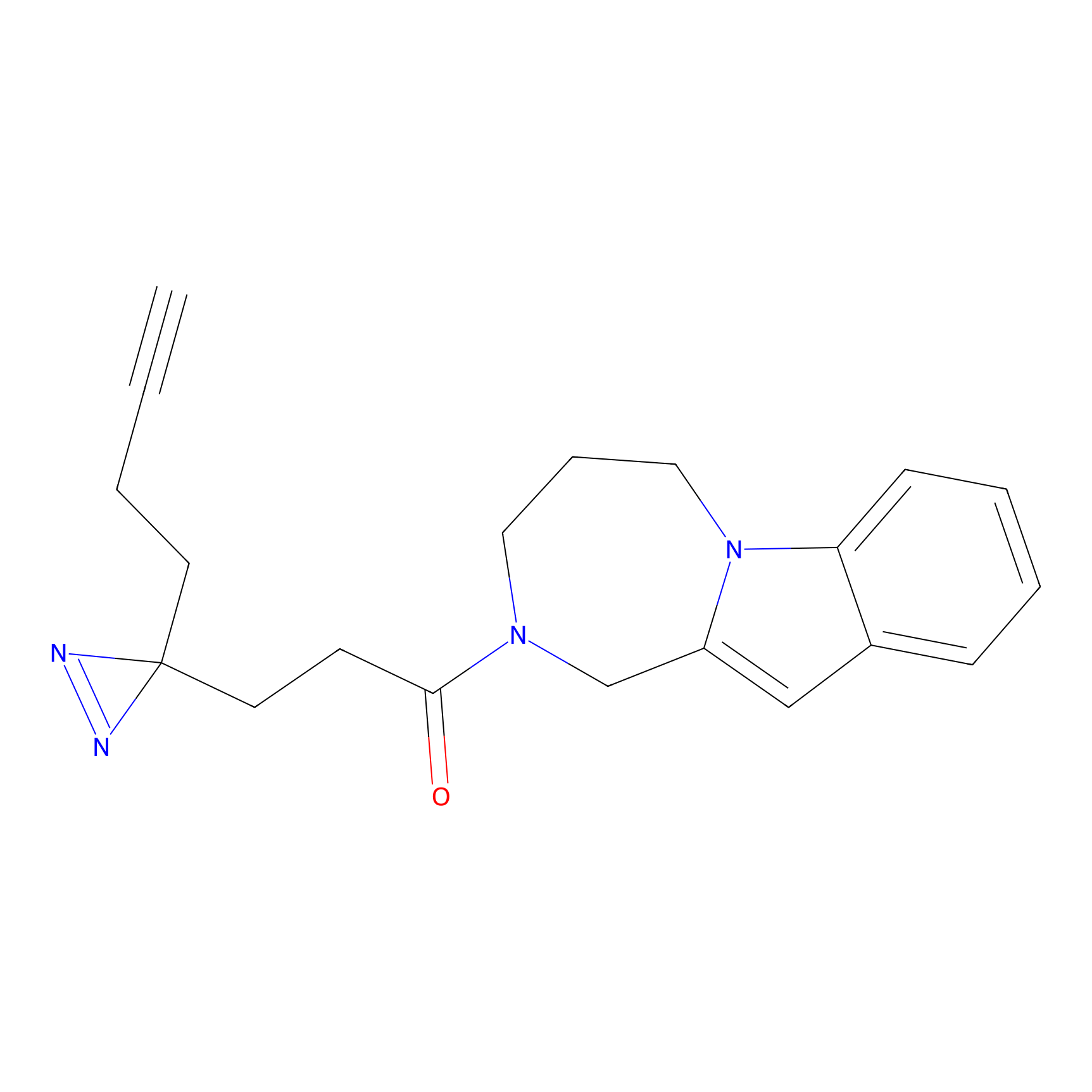
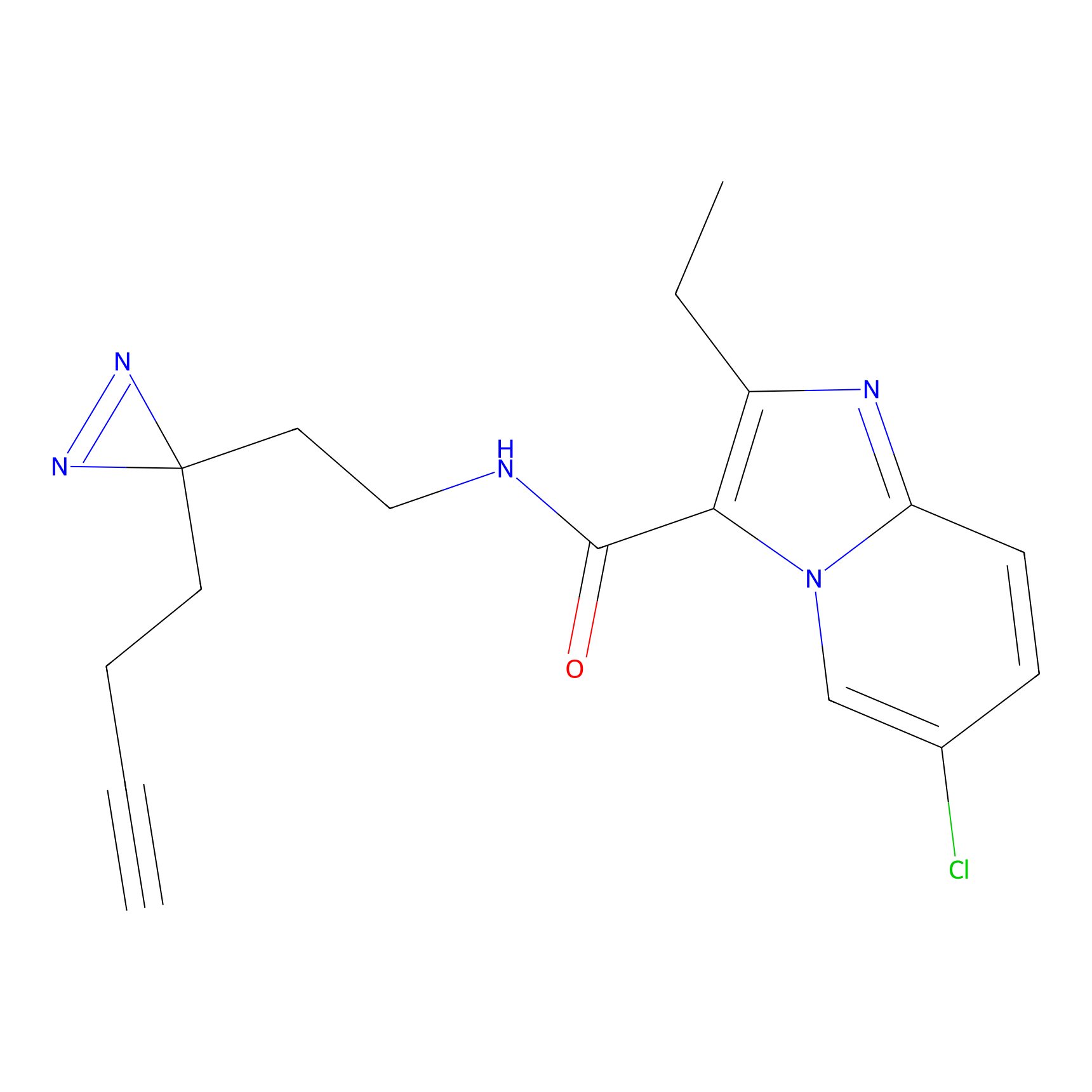
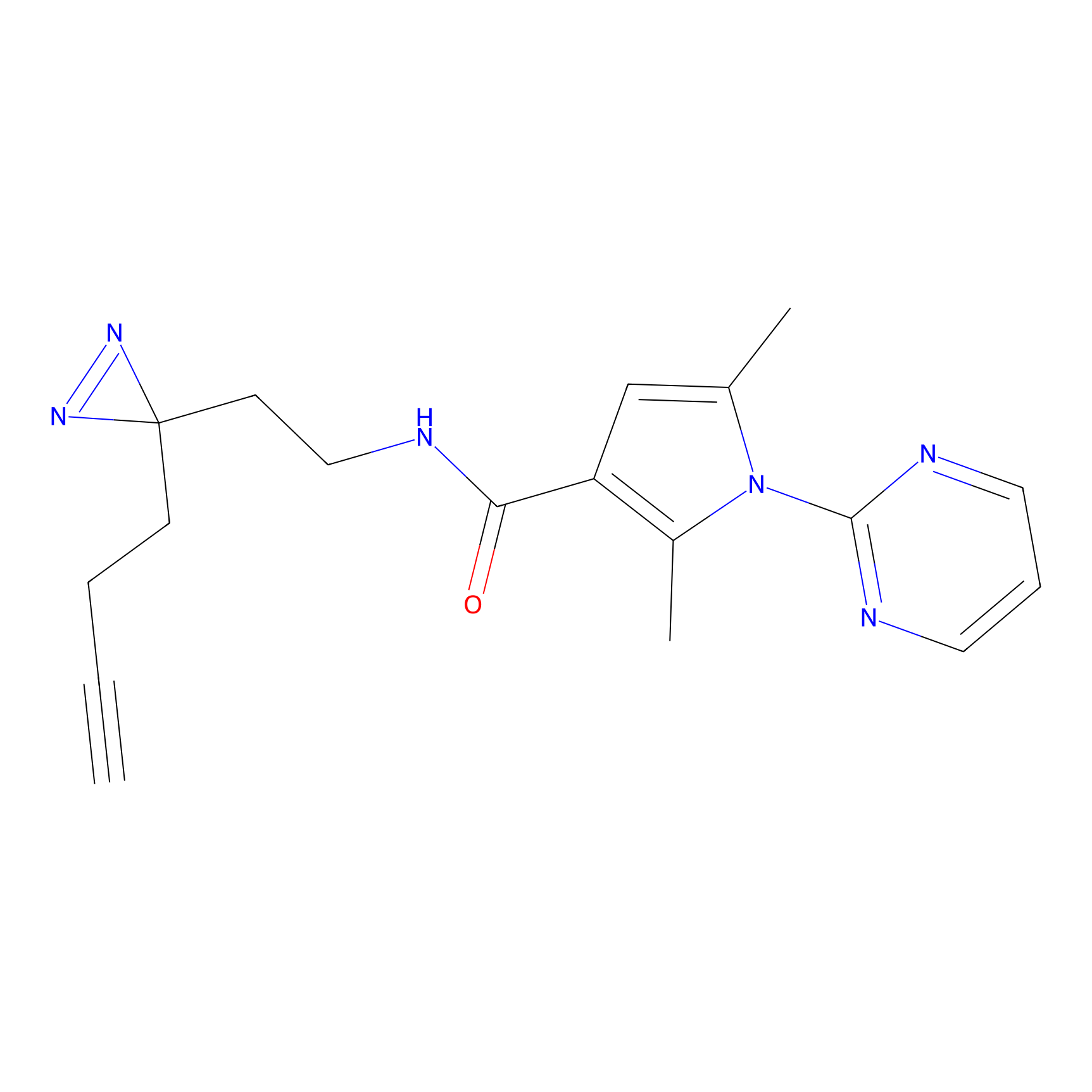
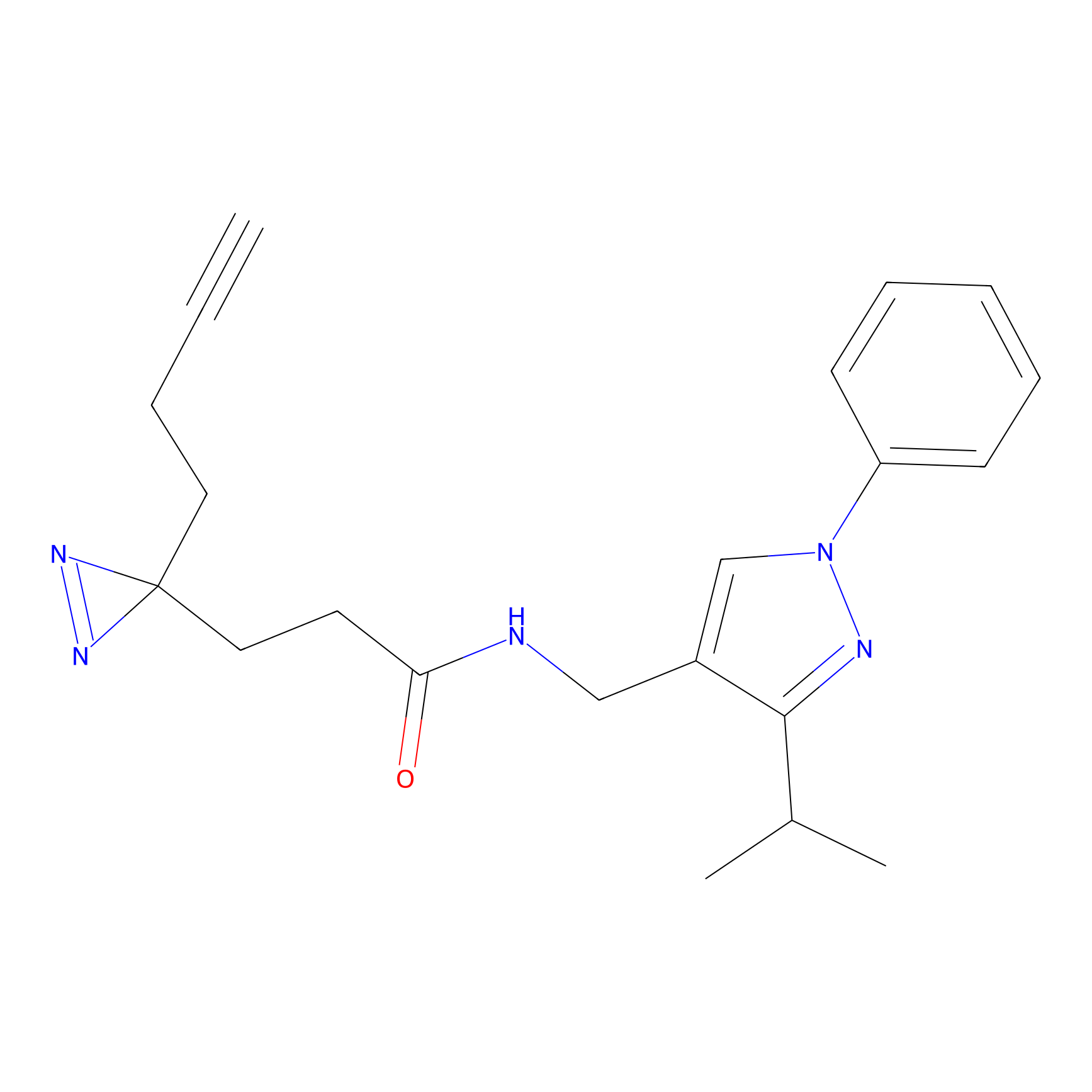
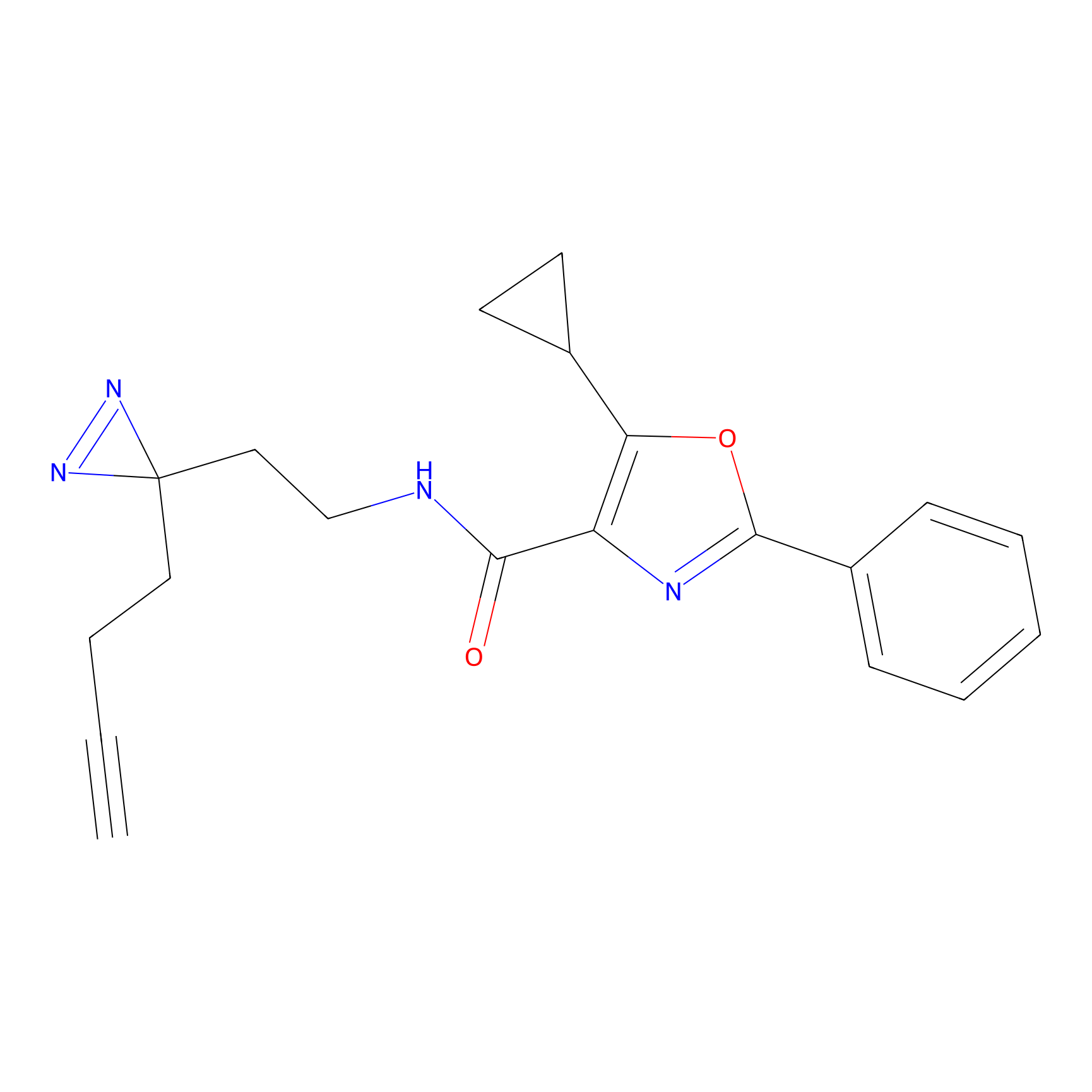
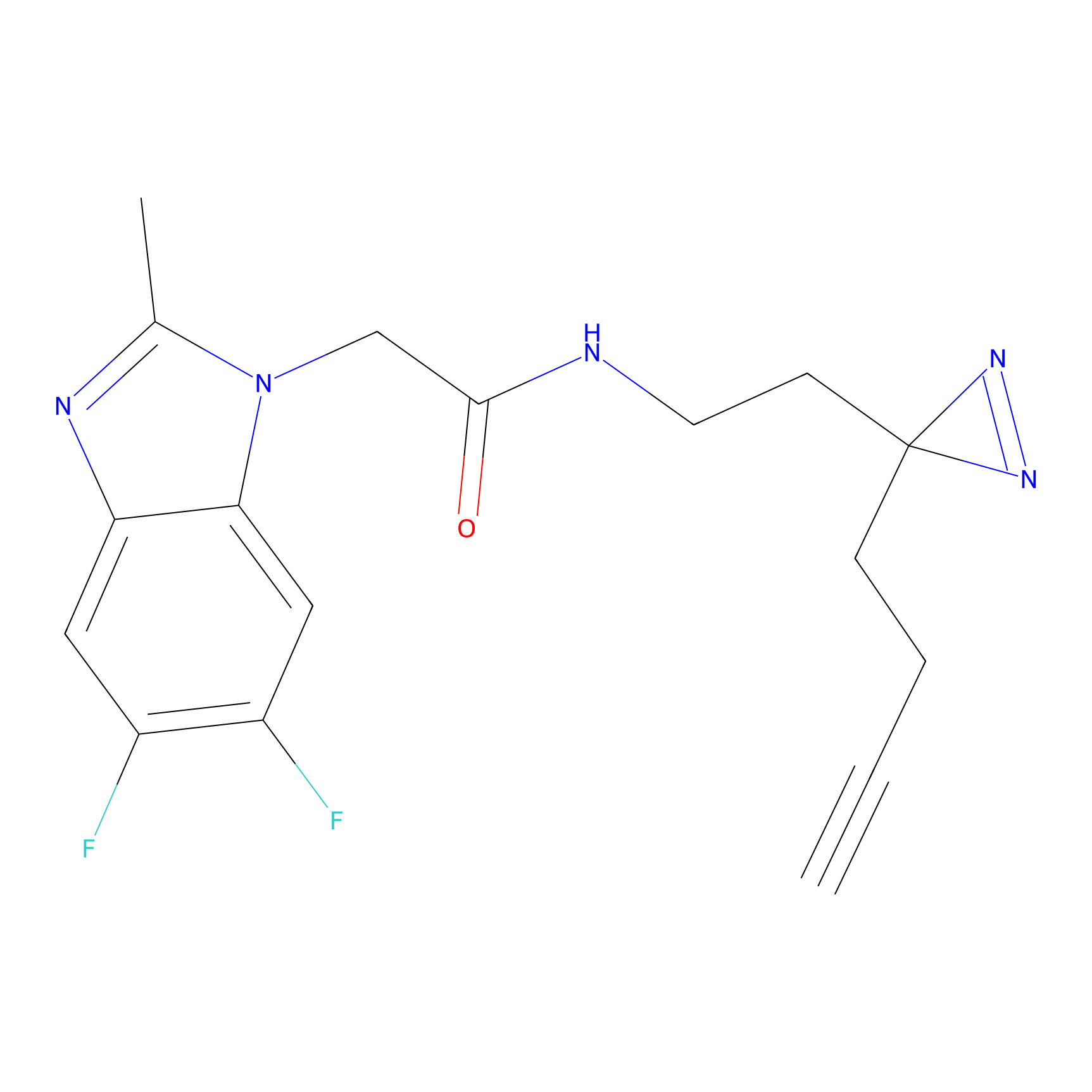
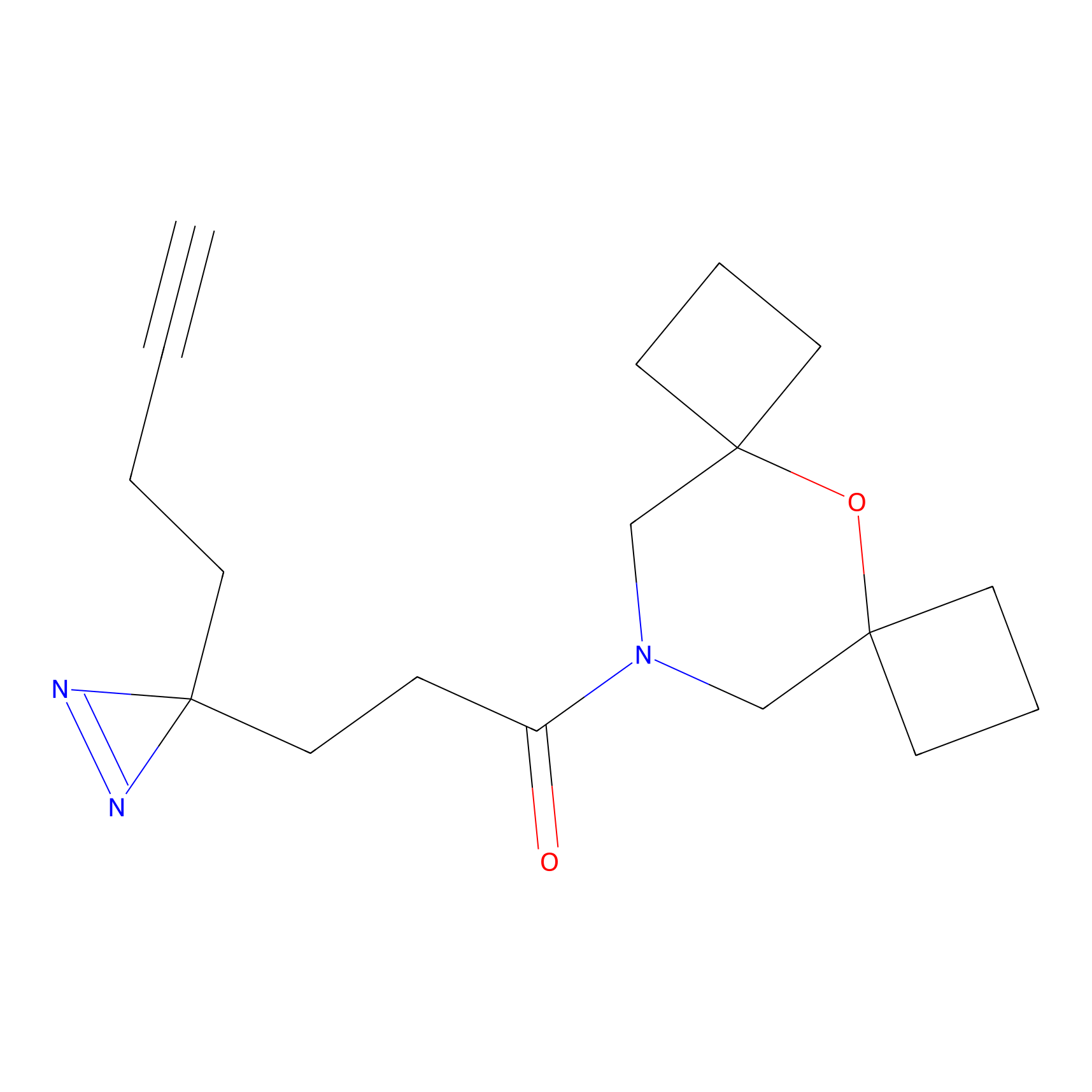
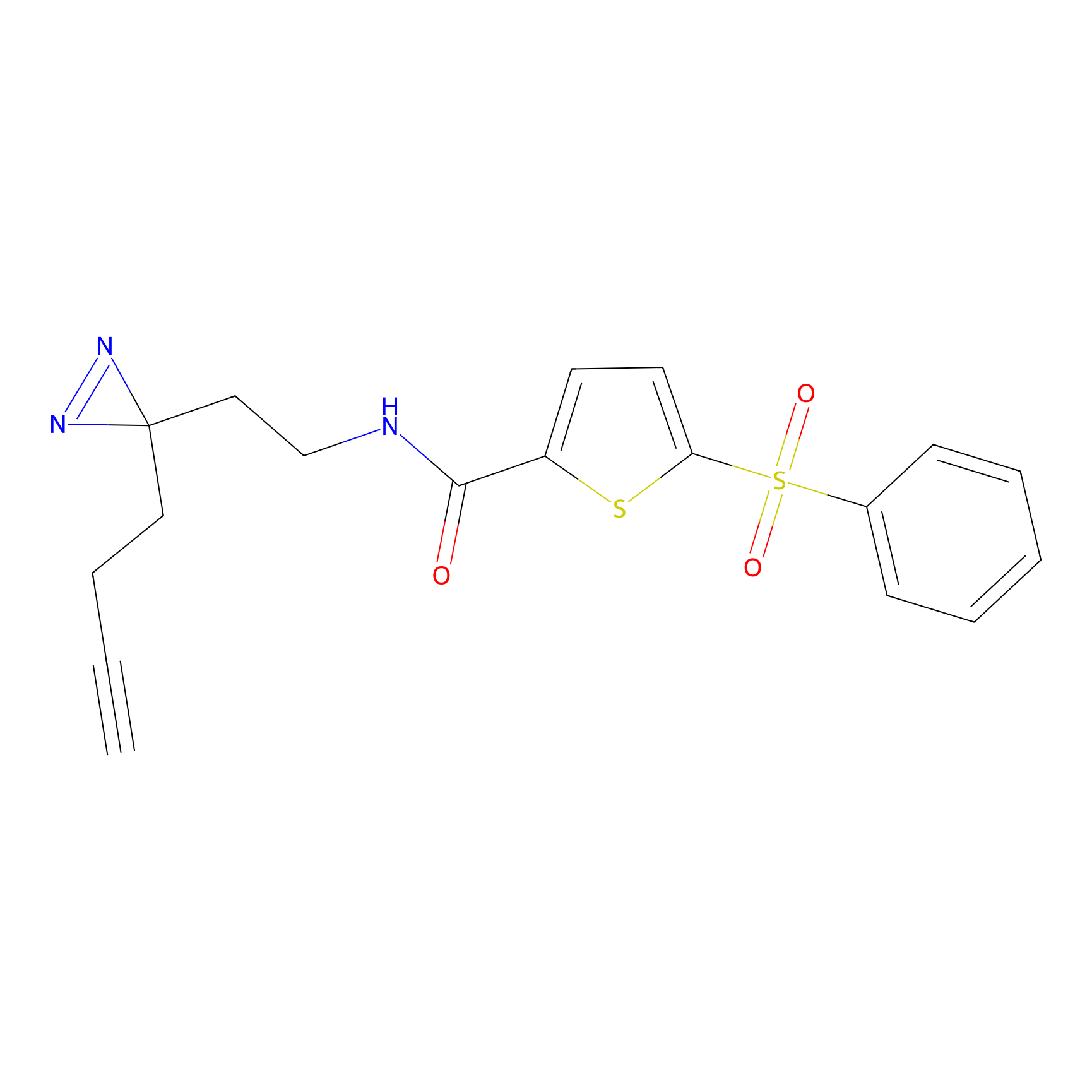
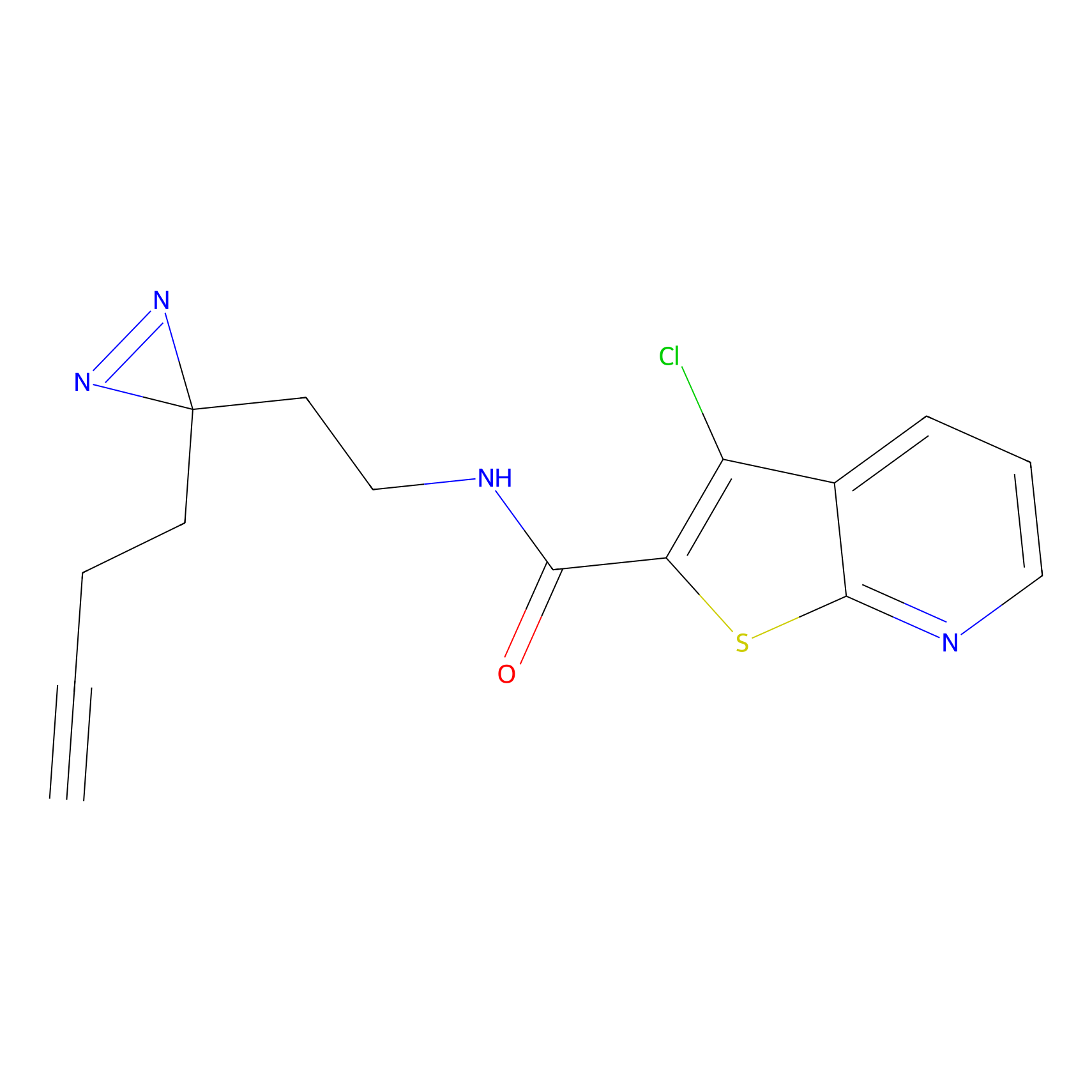
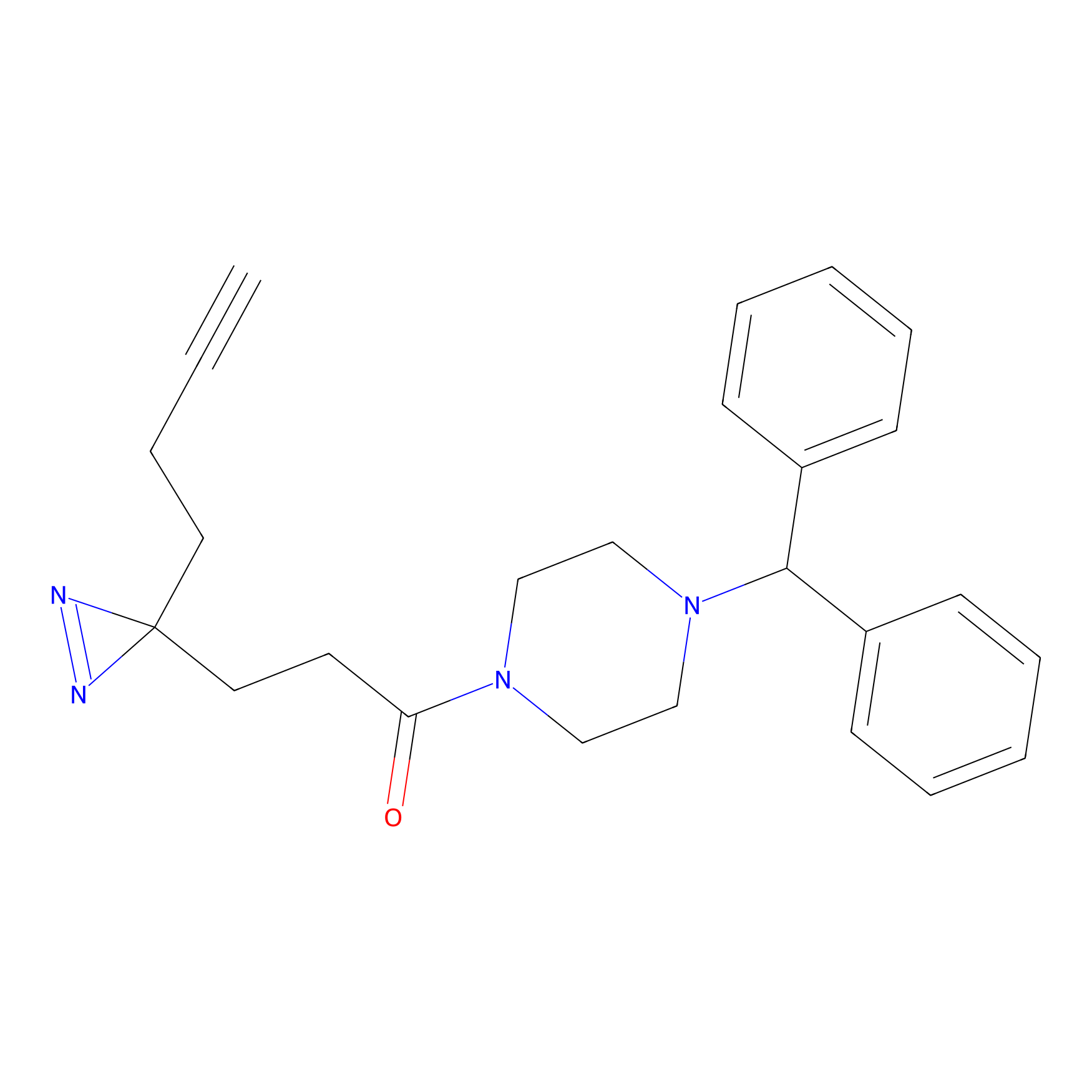
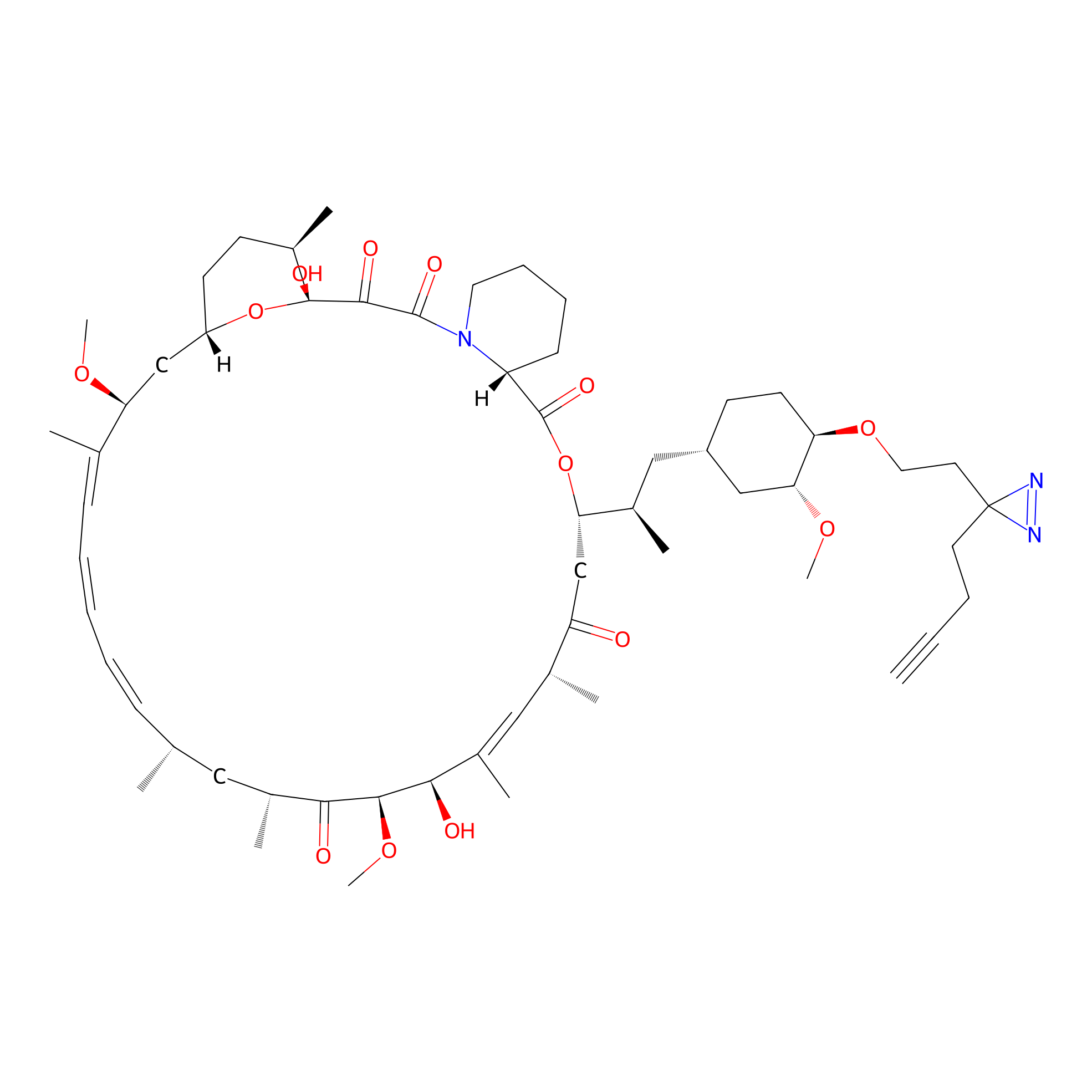
|
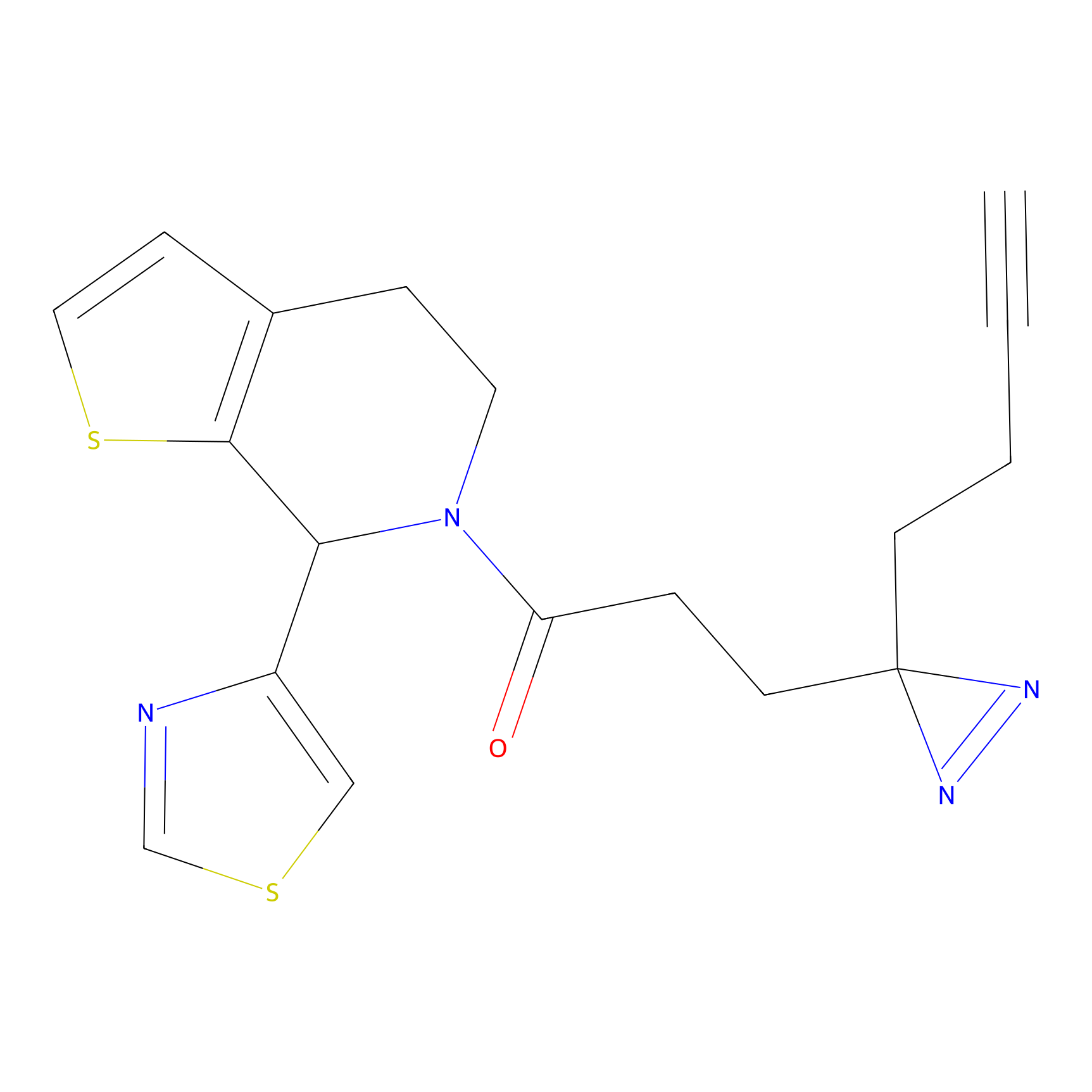
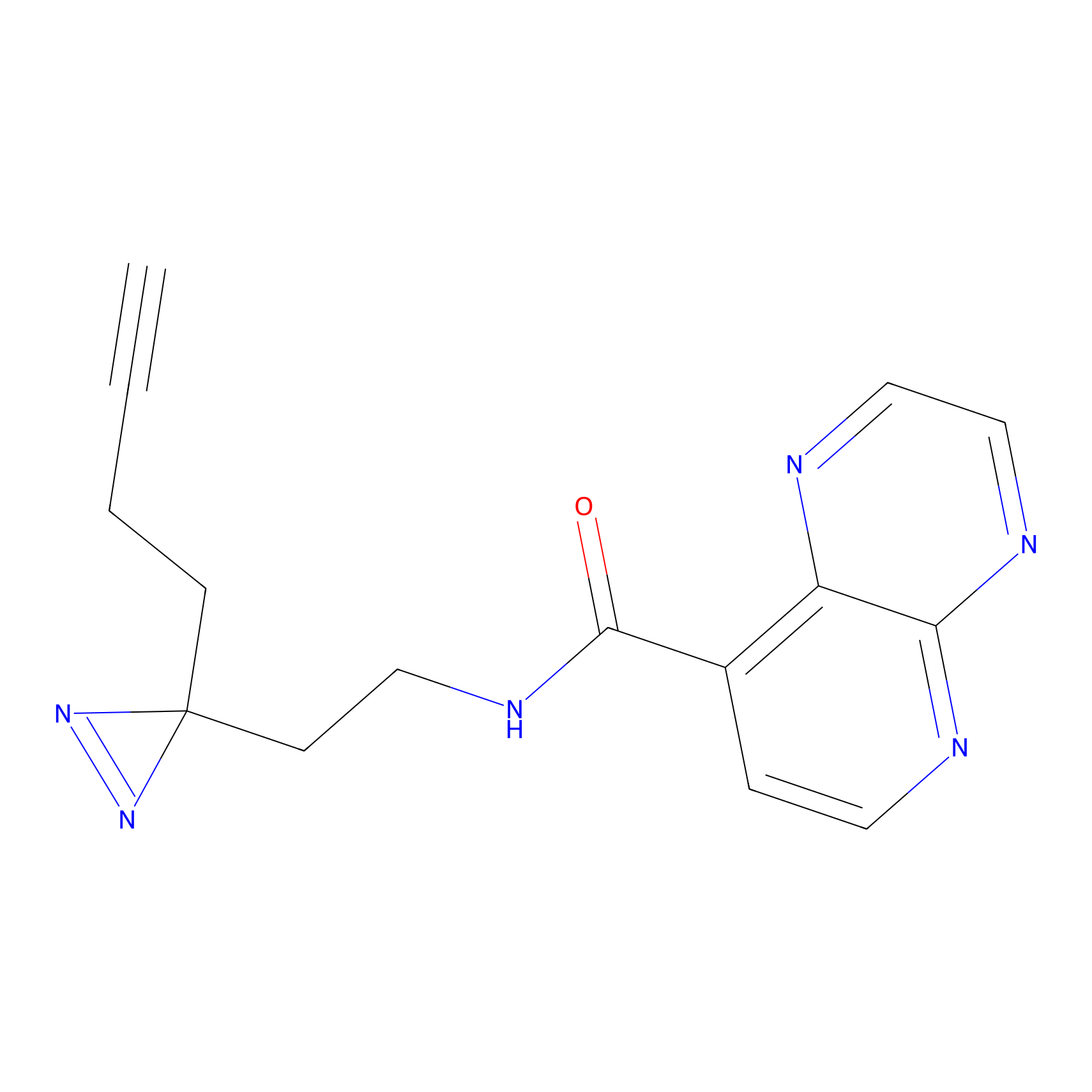
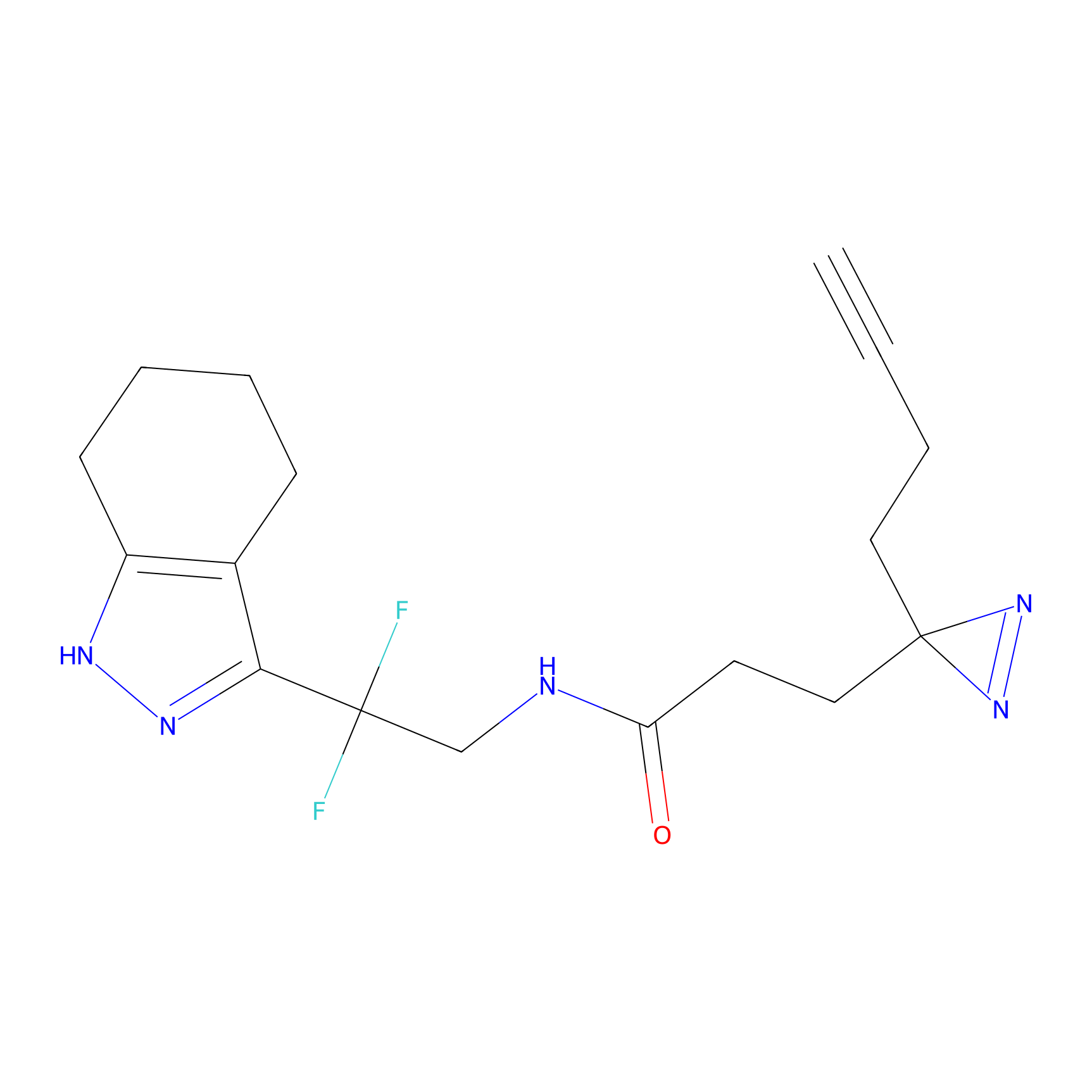
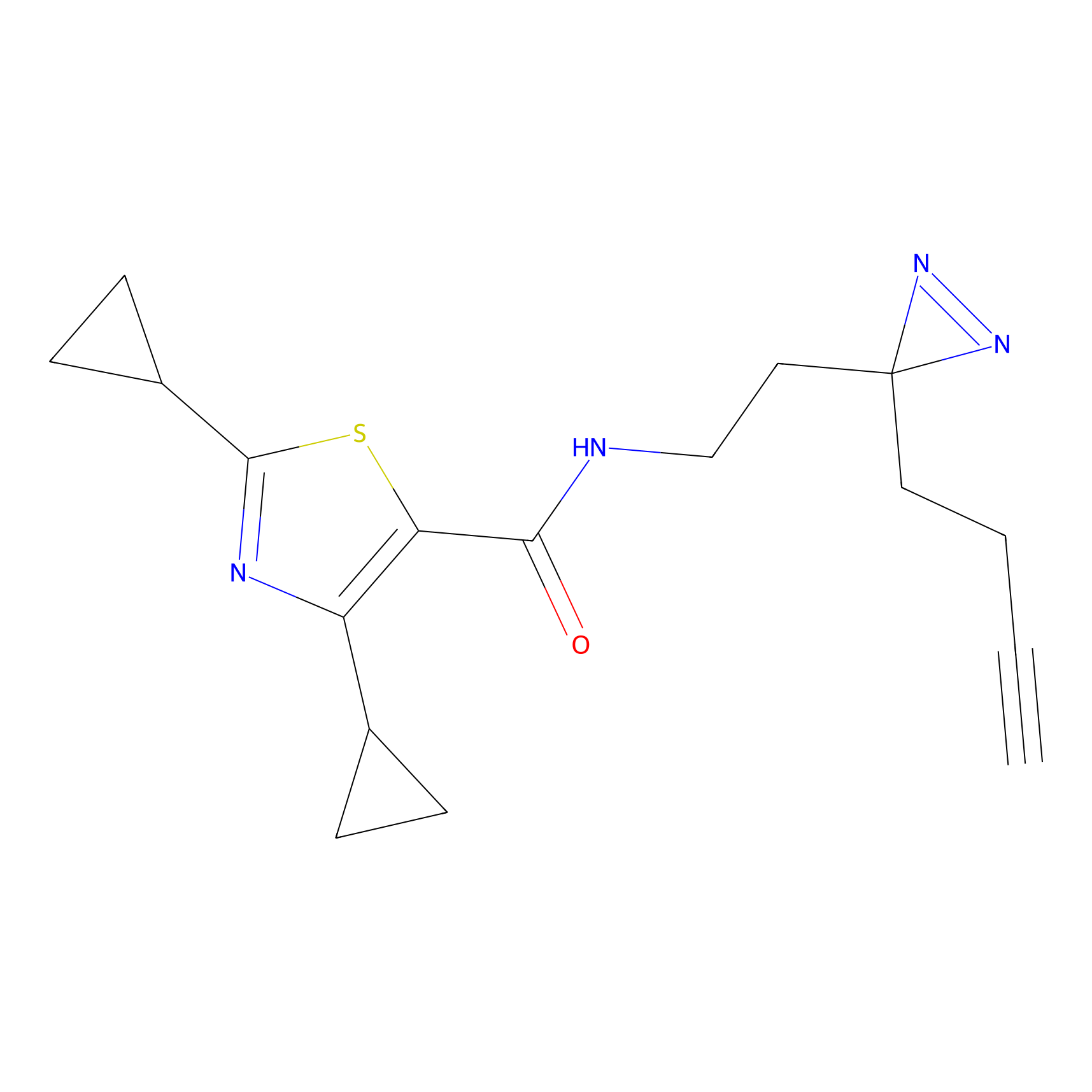
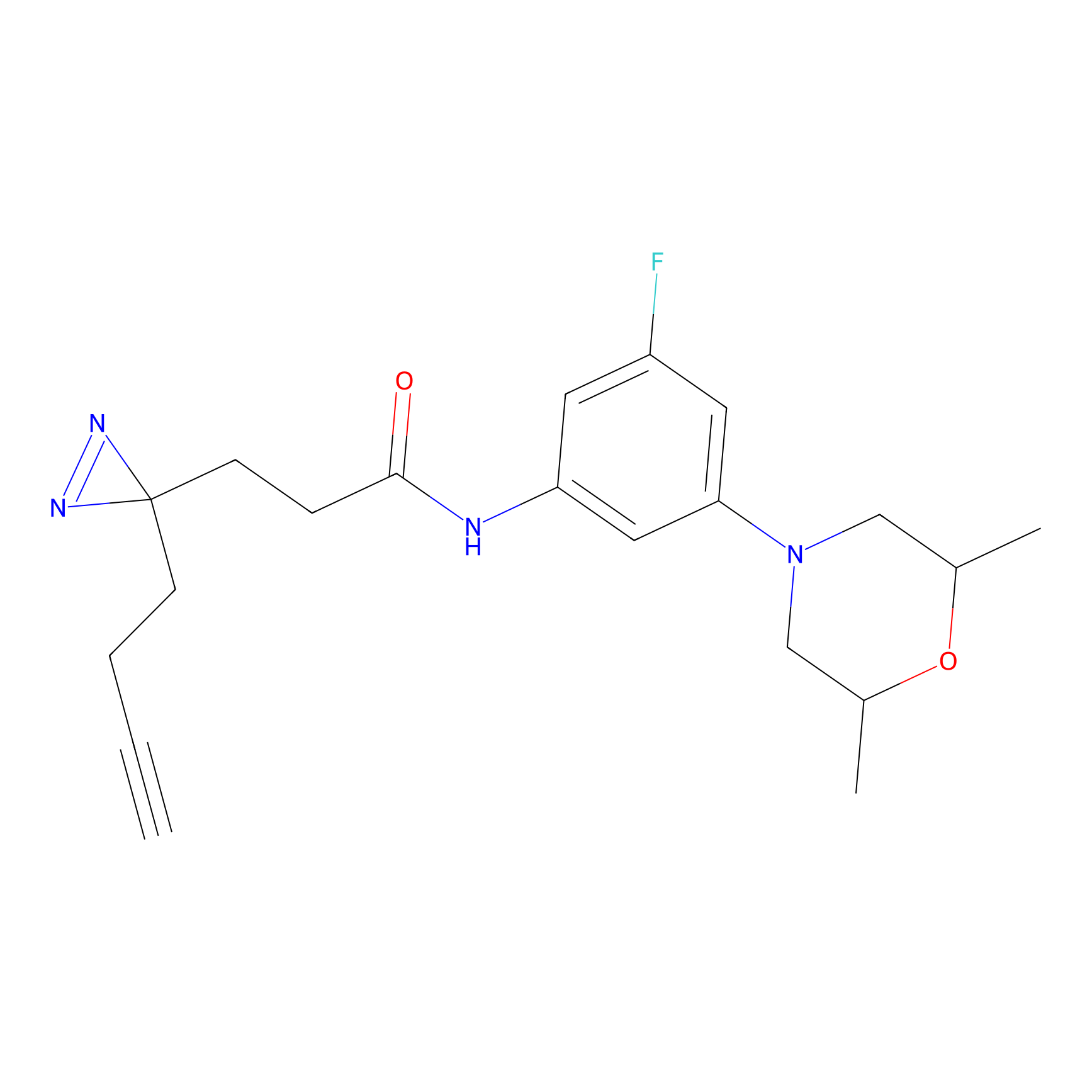
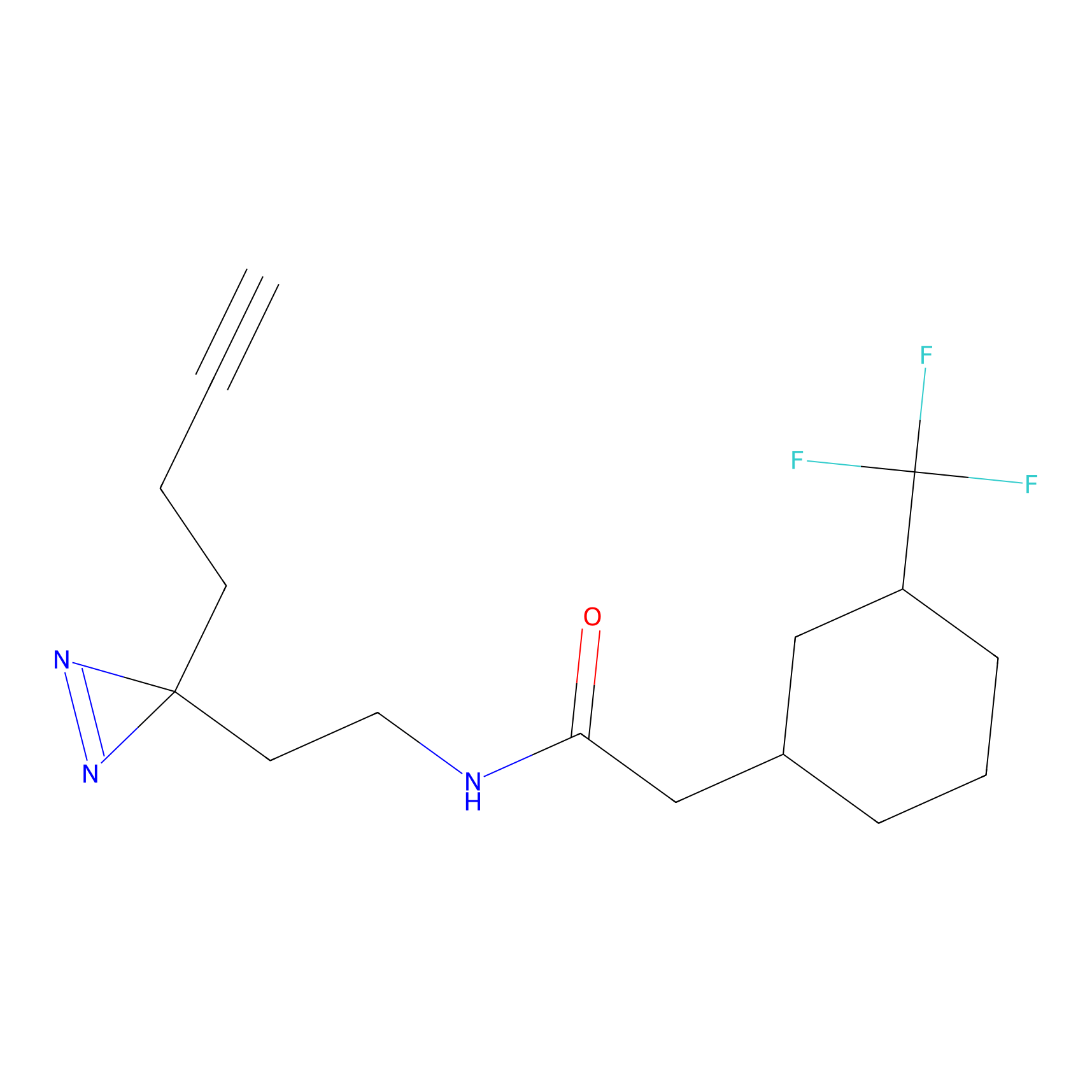
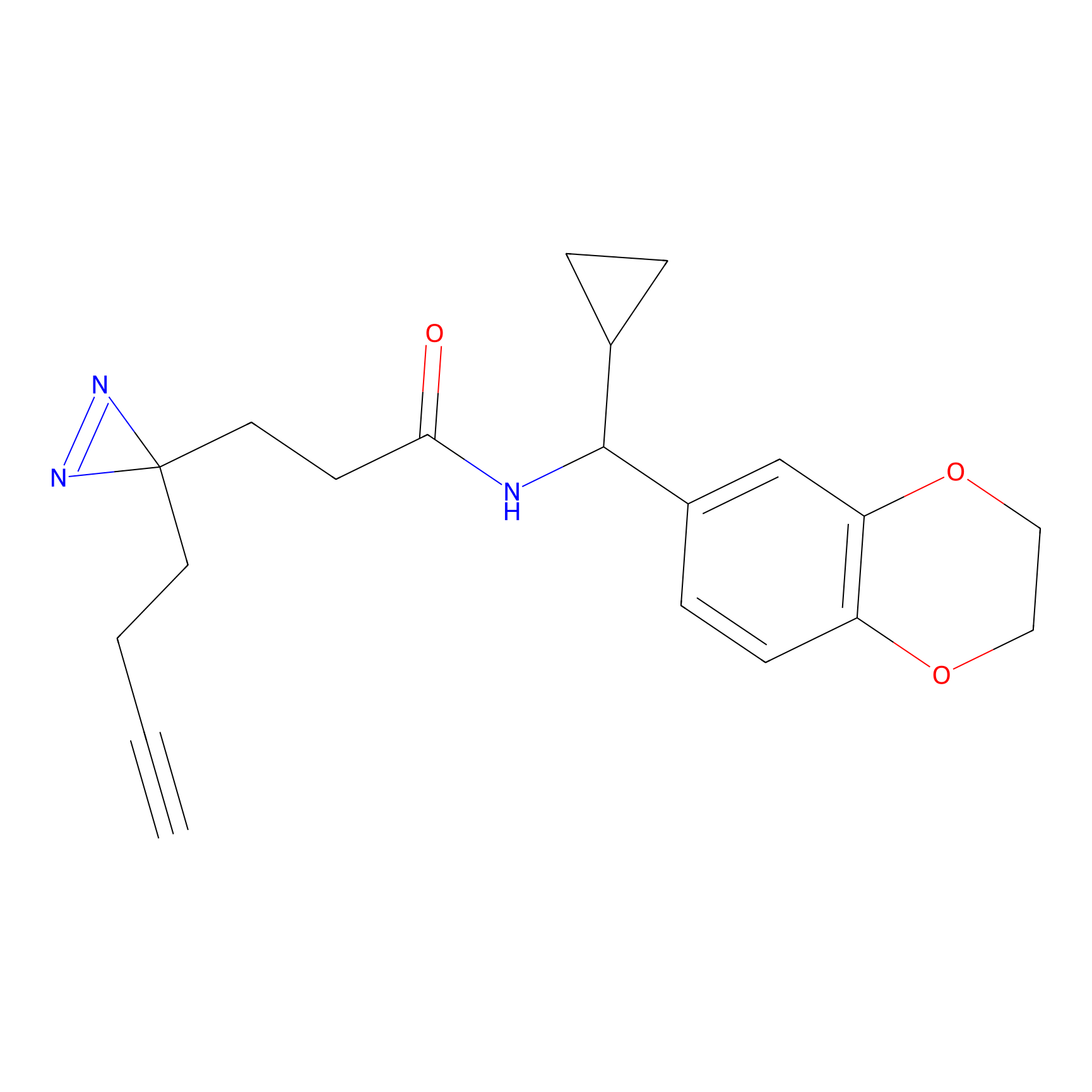
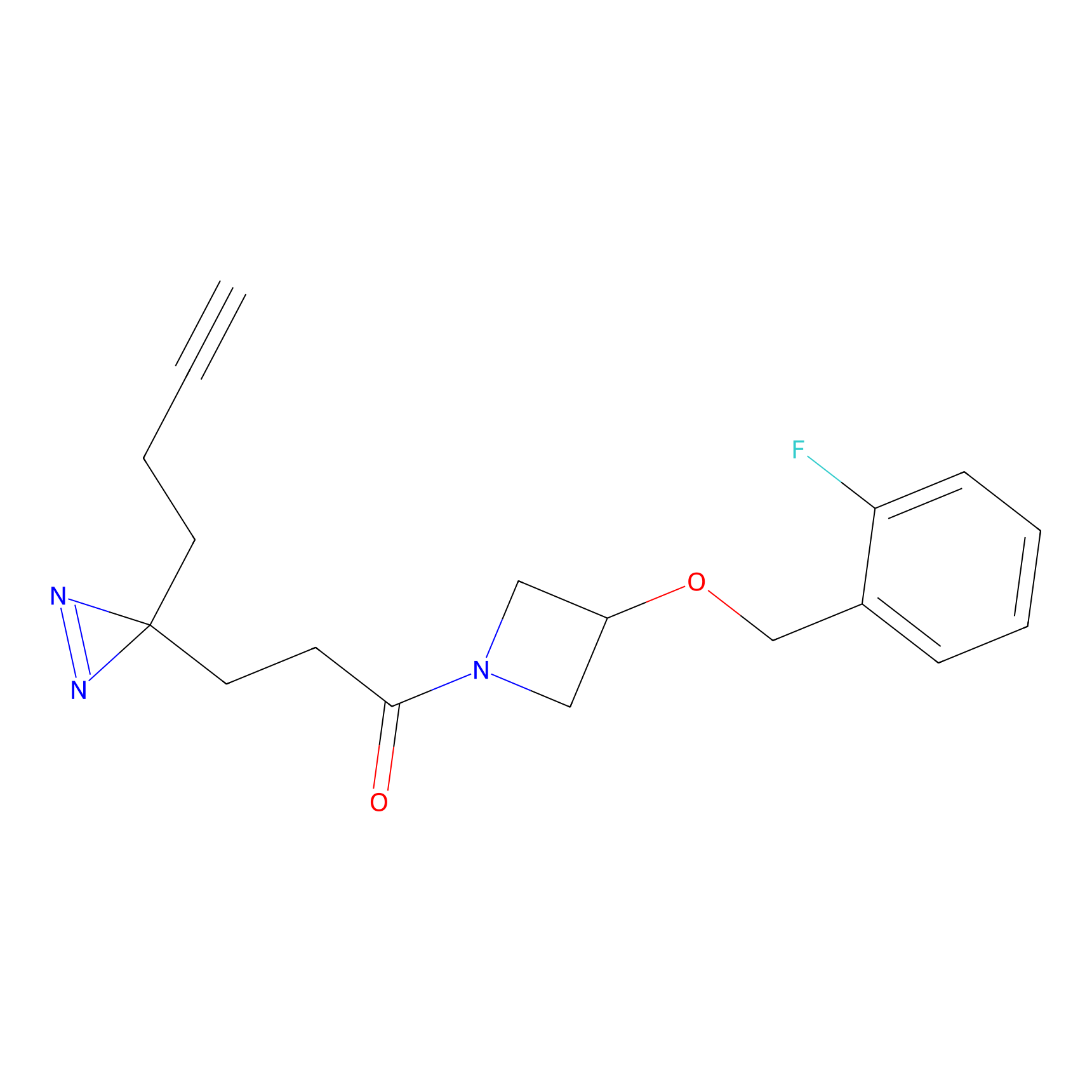
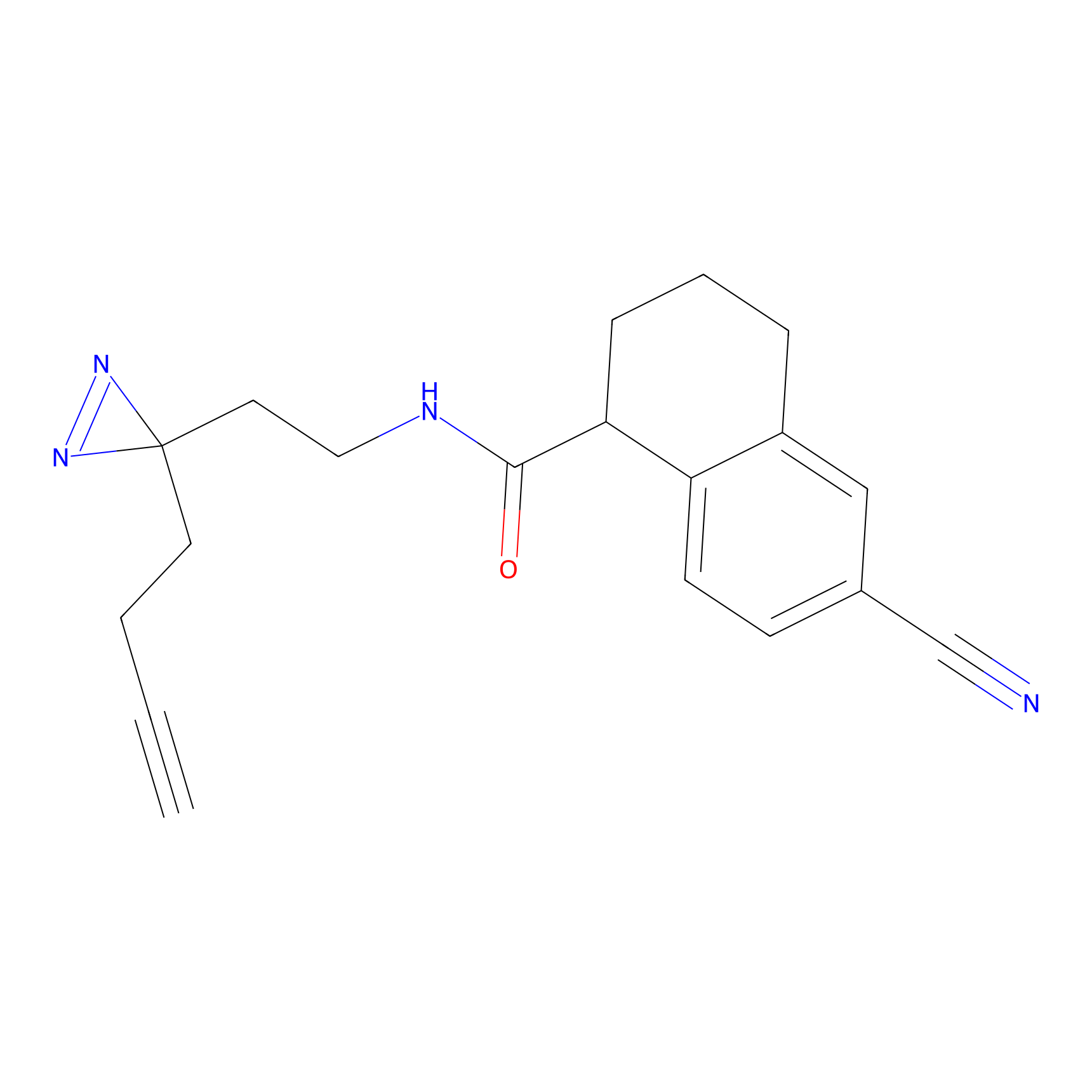
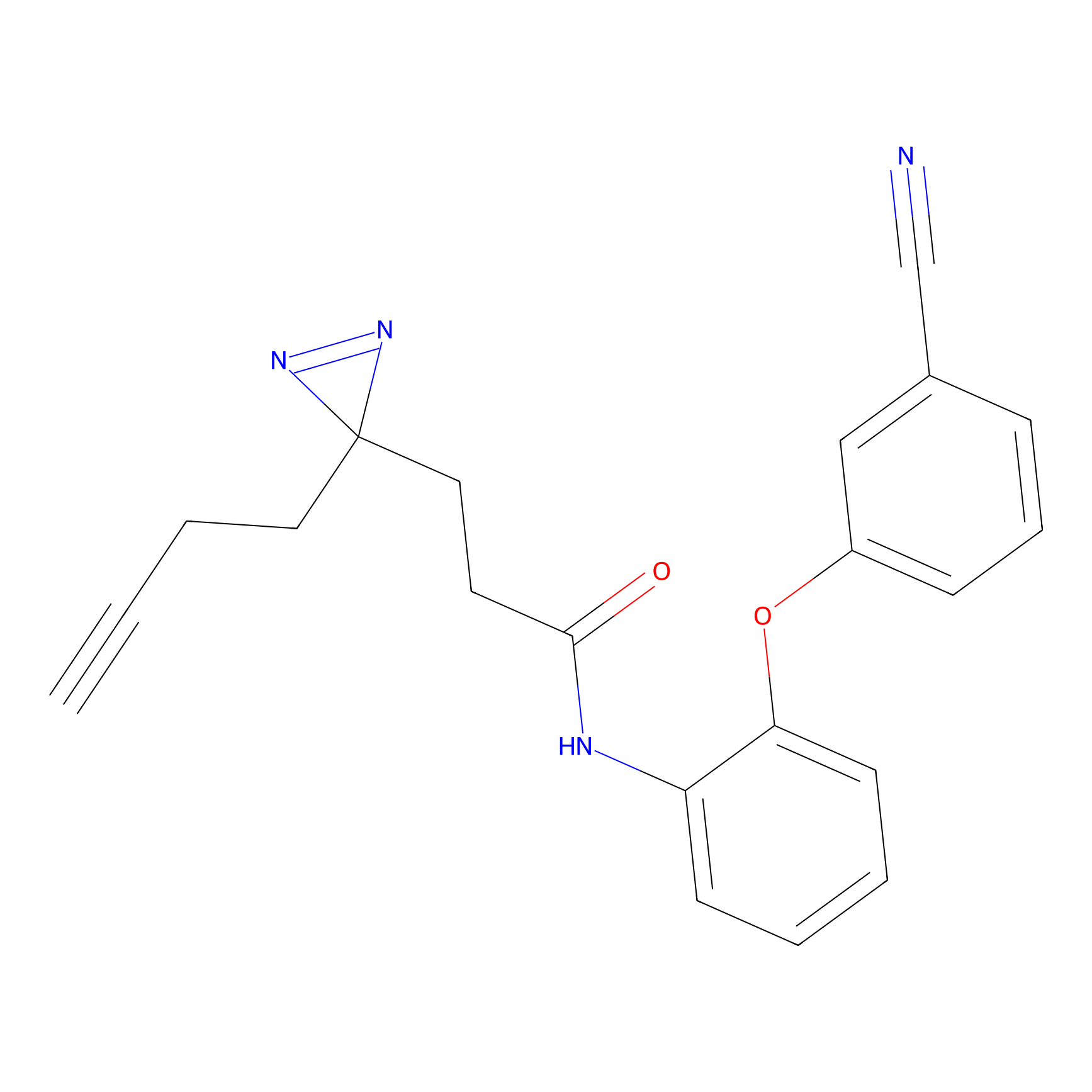
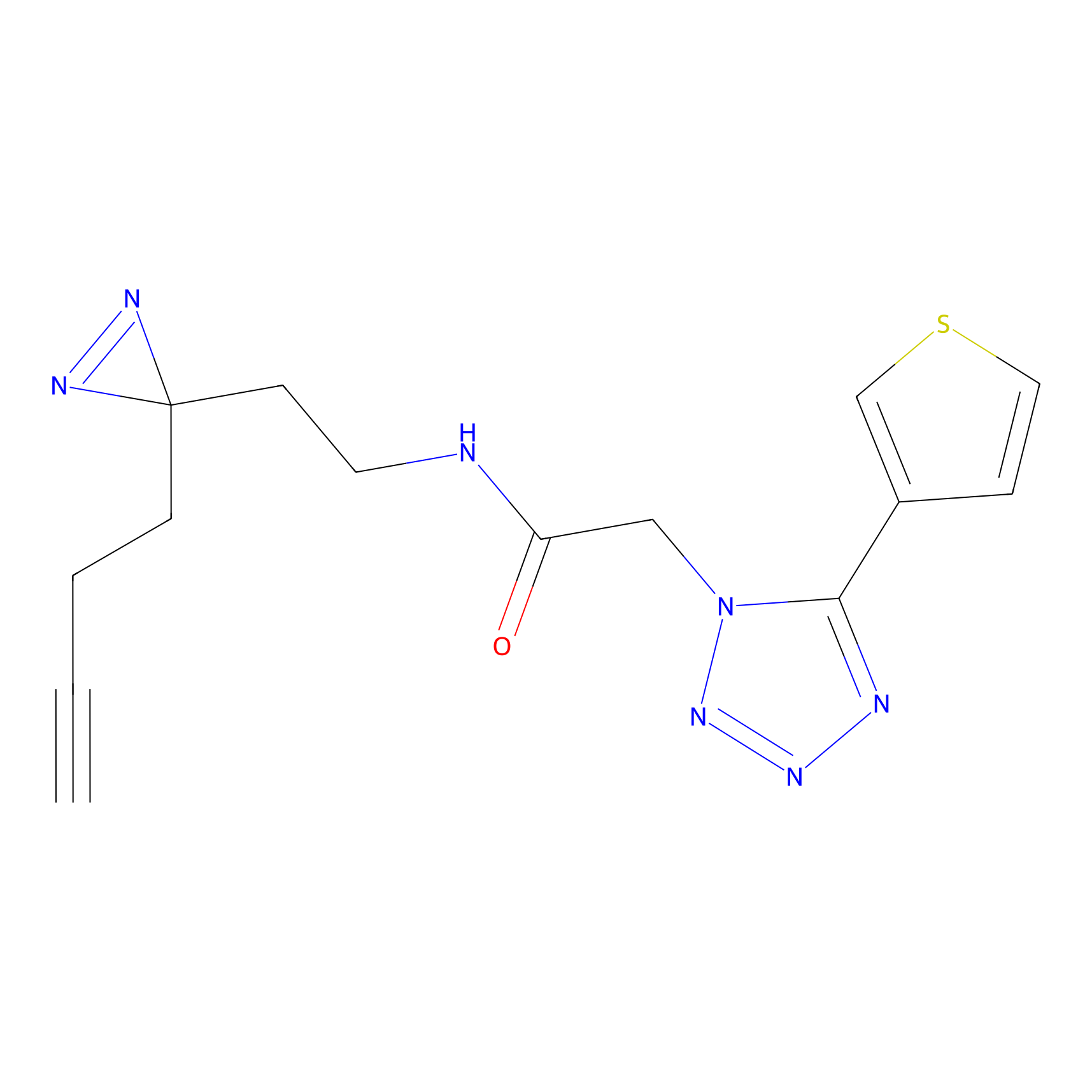
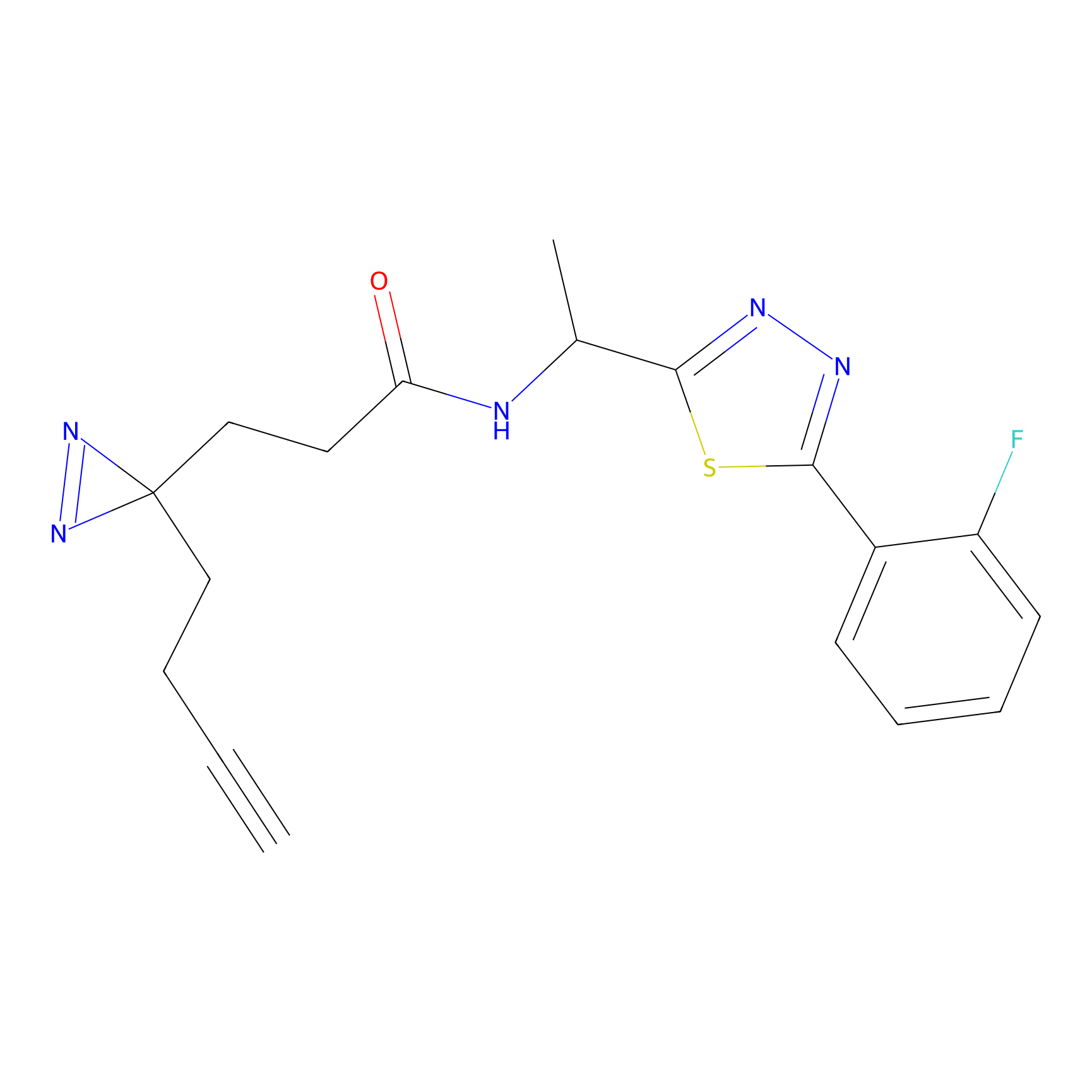
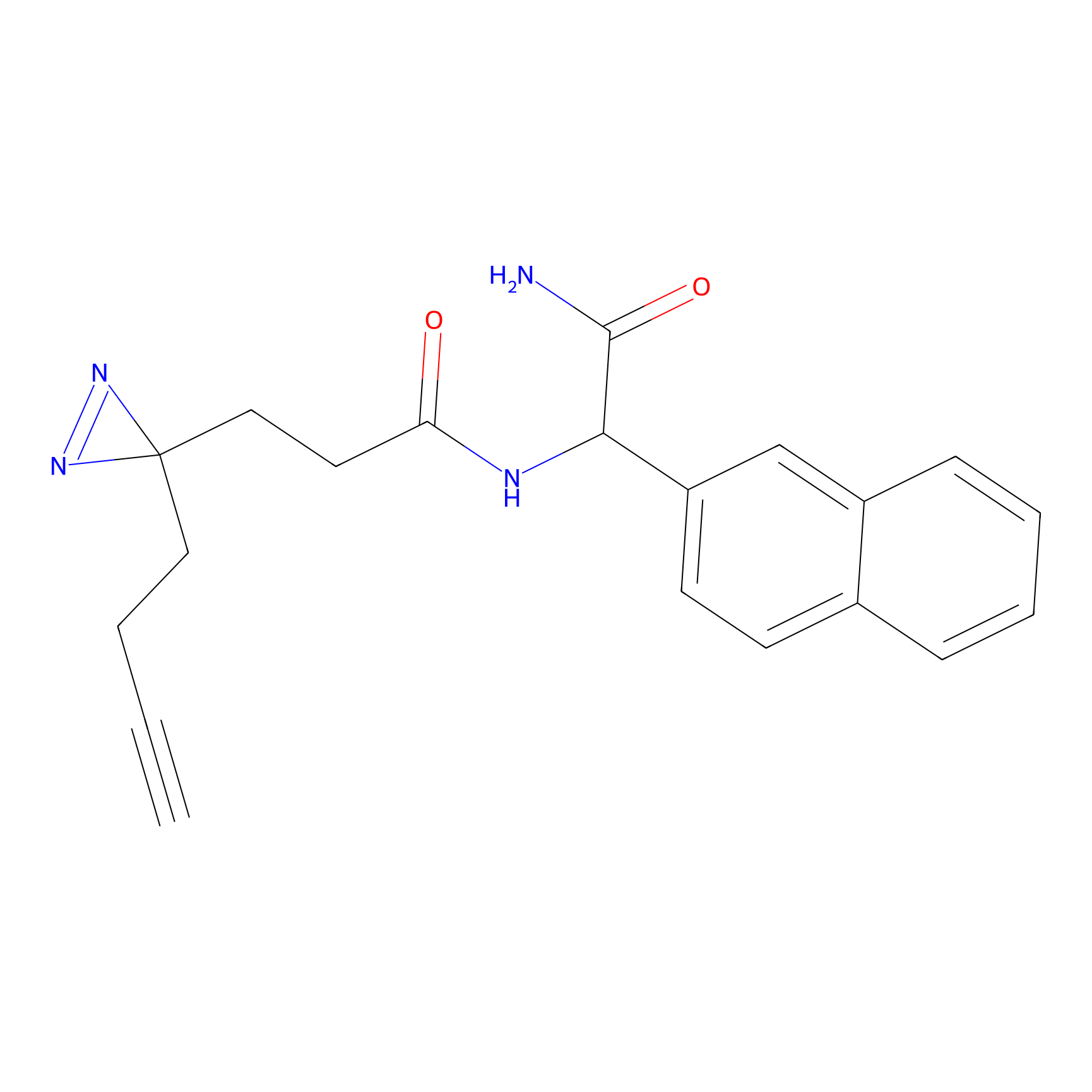
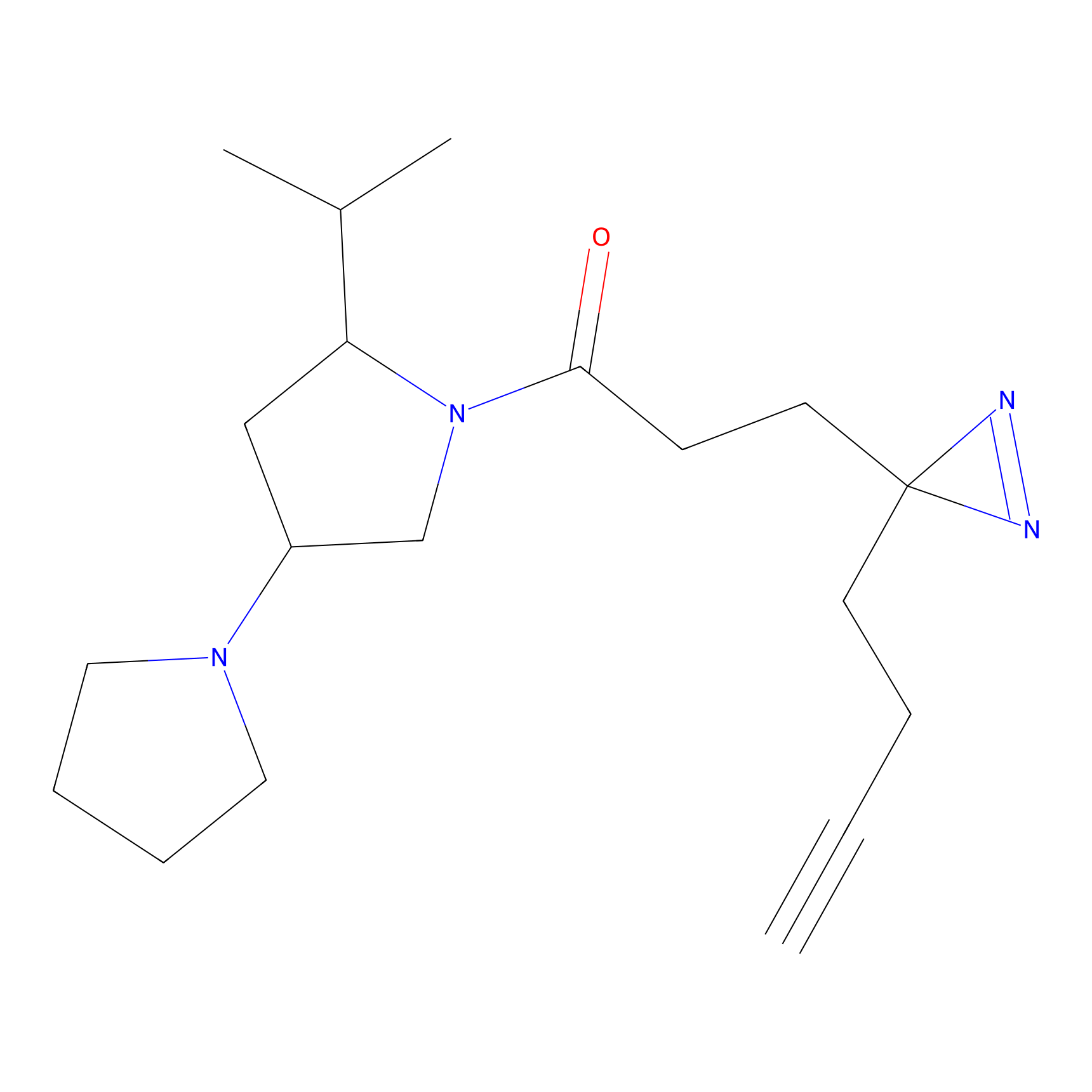
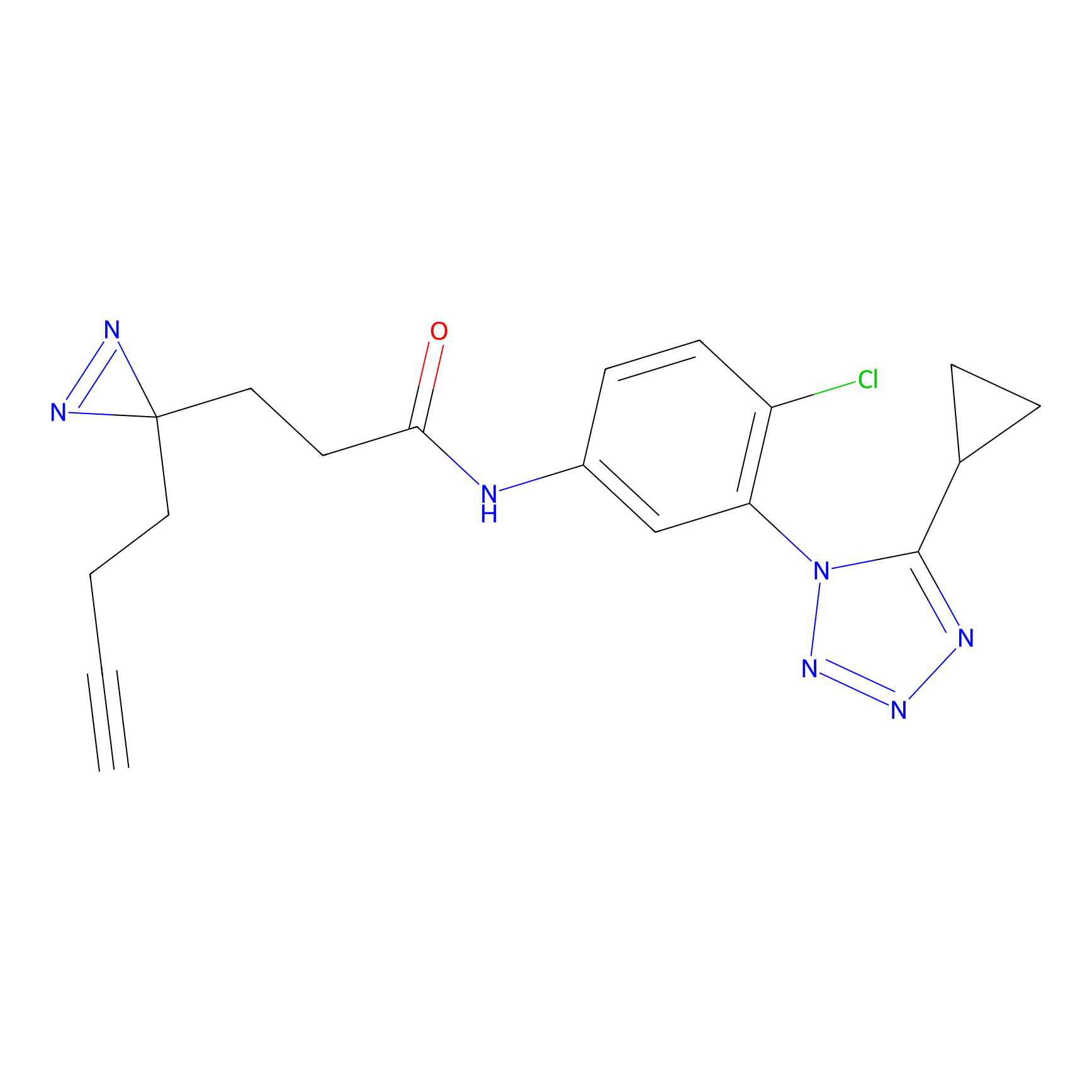
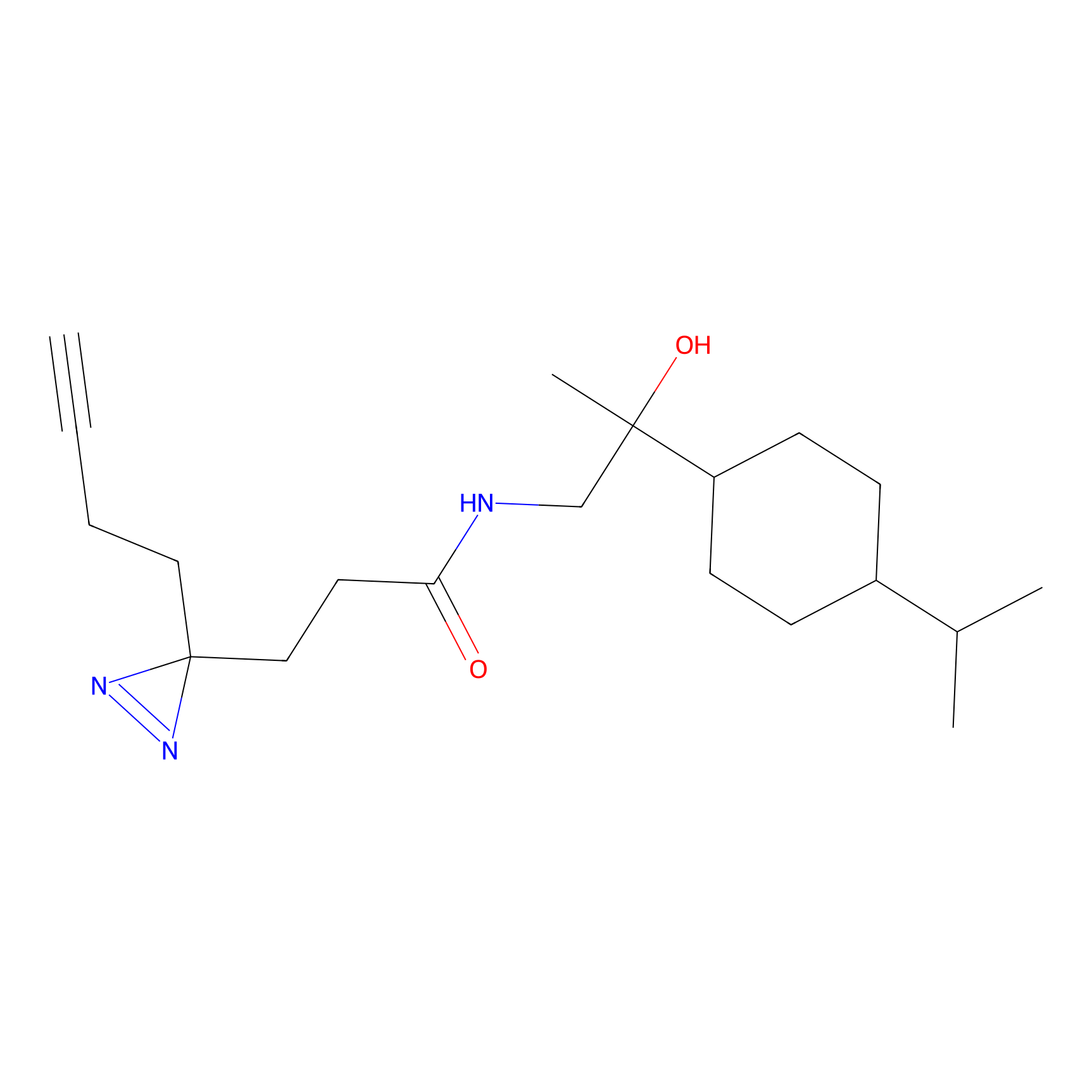
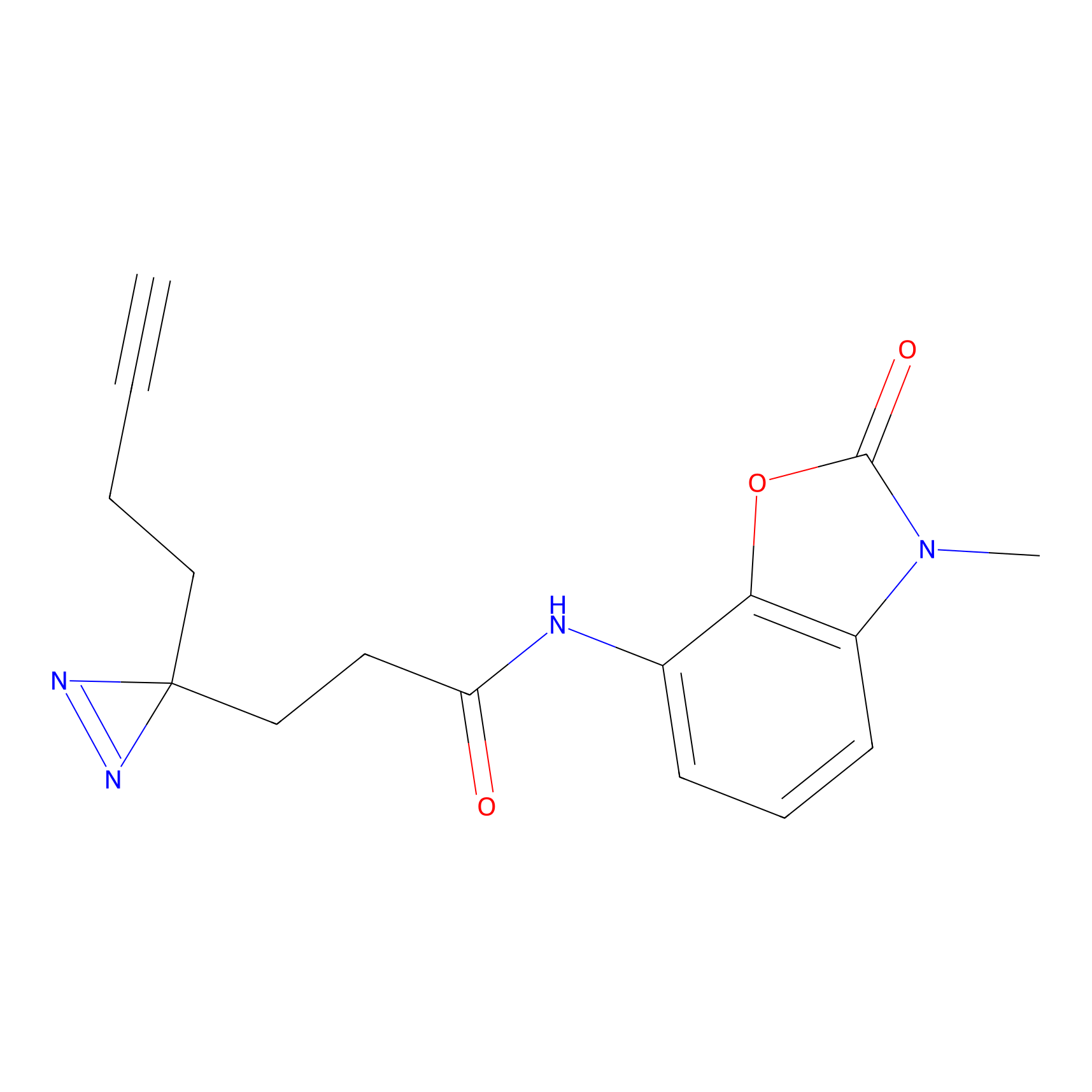
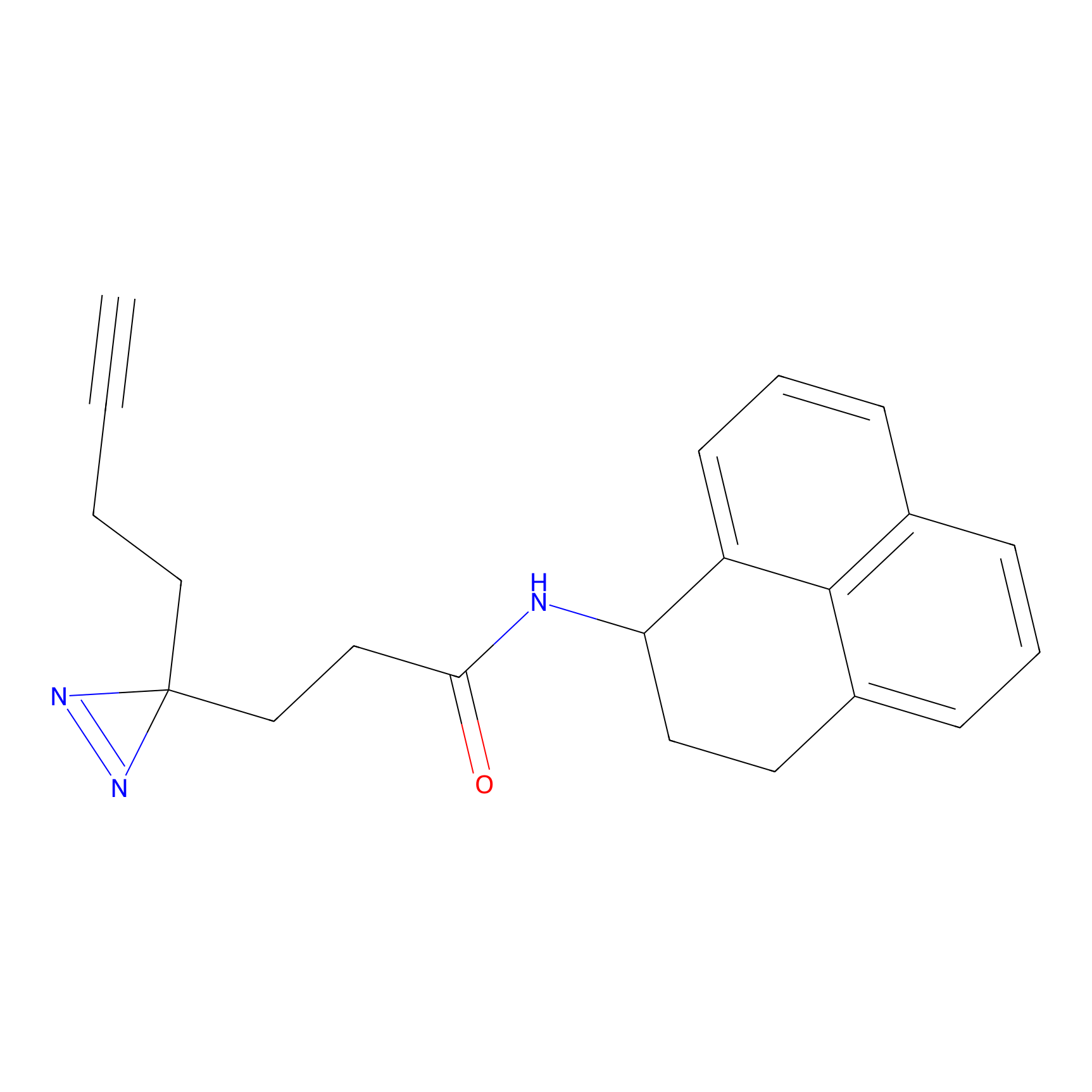
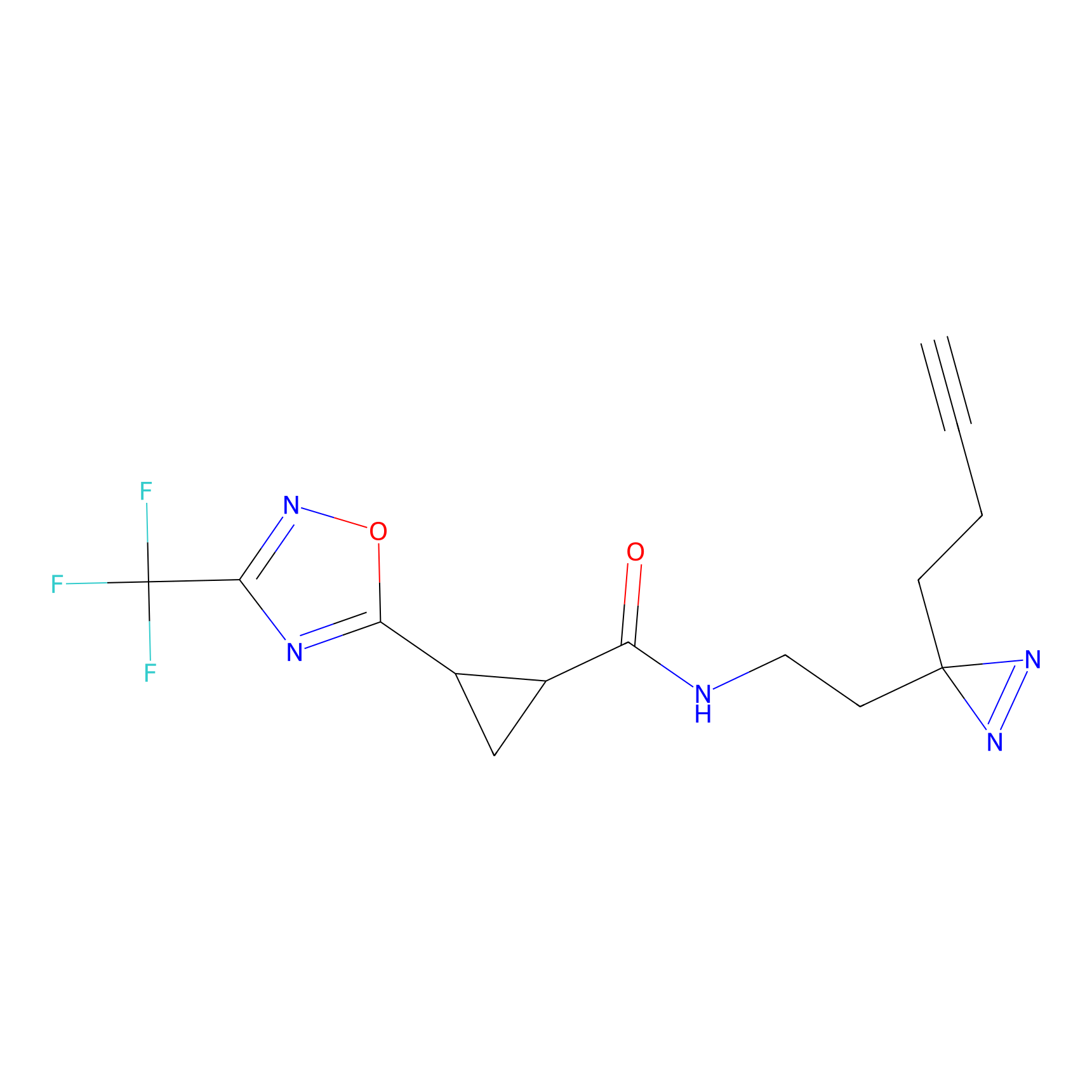
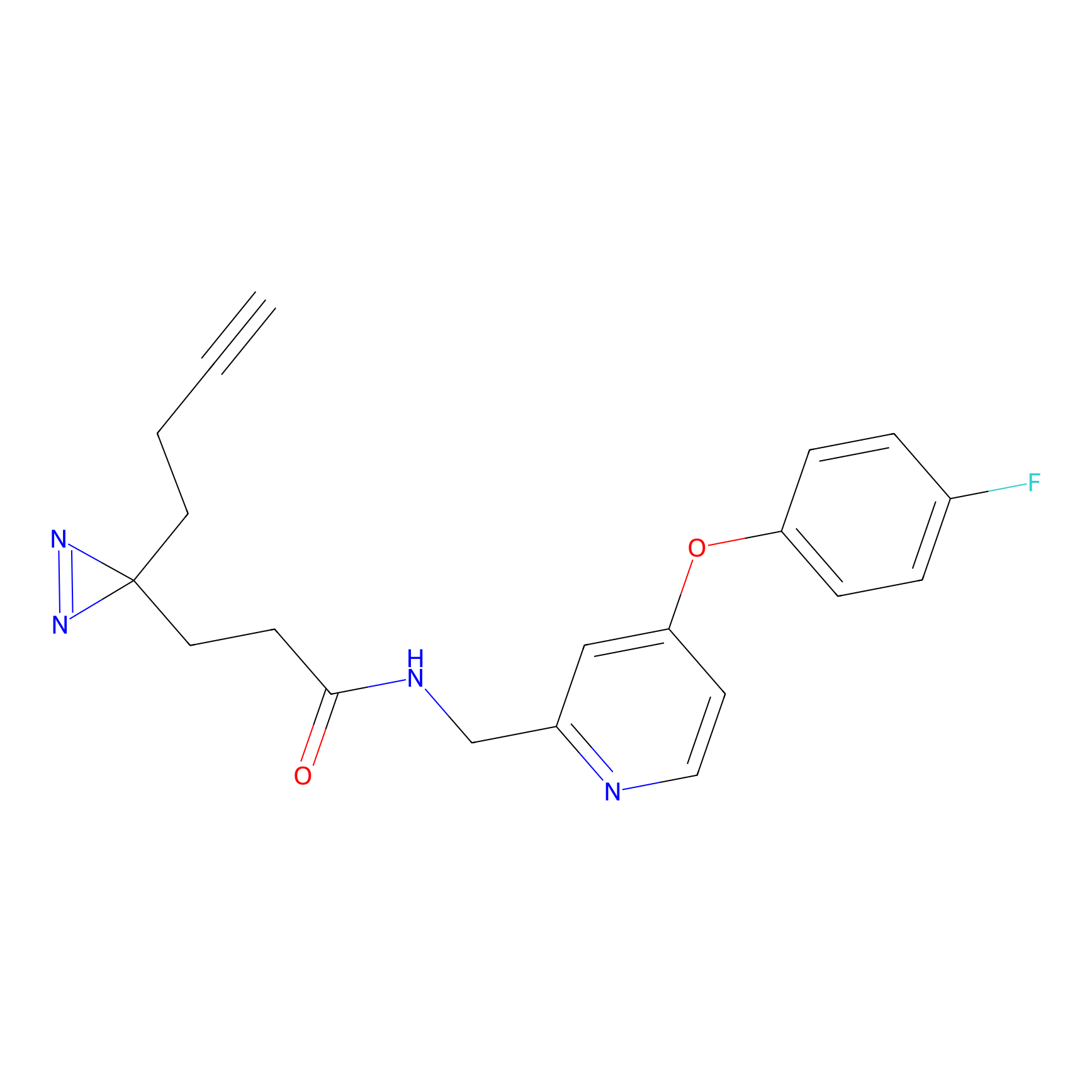
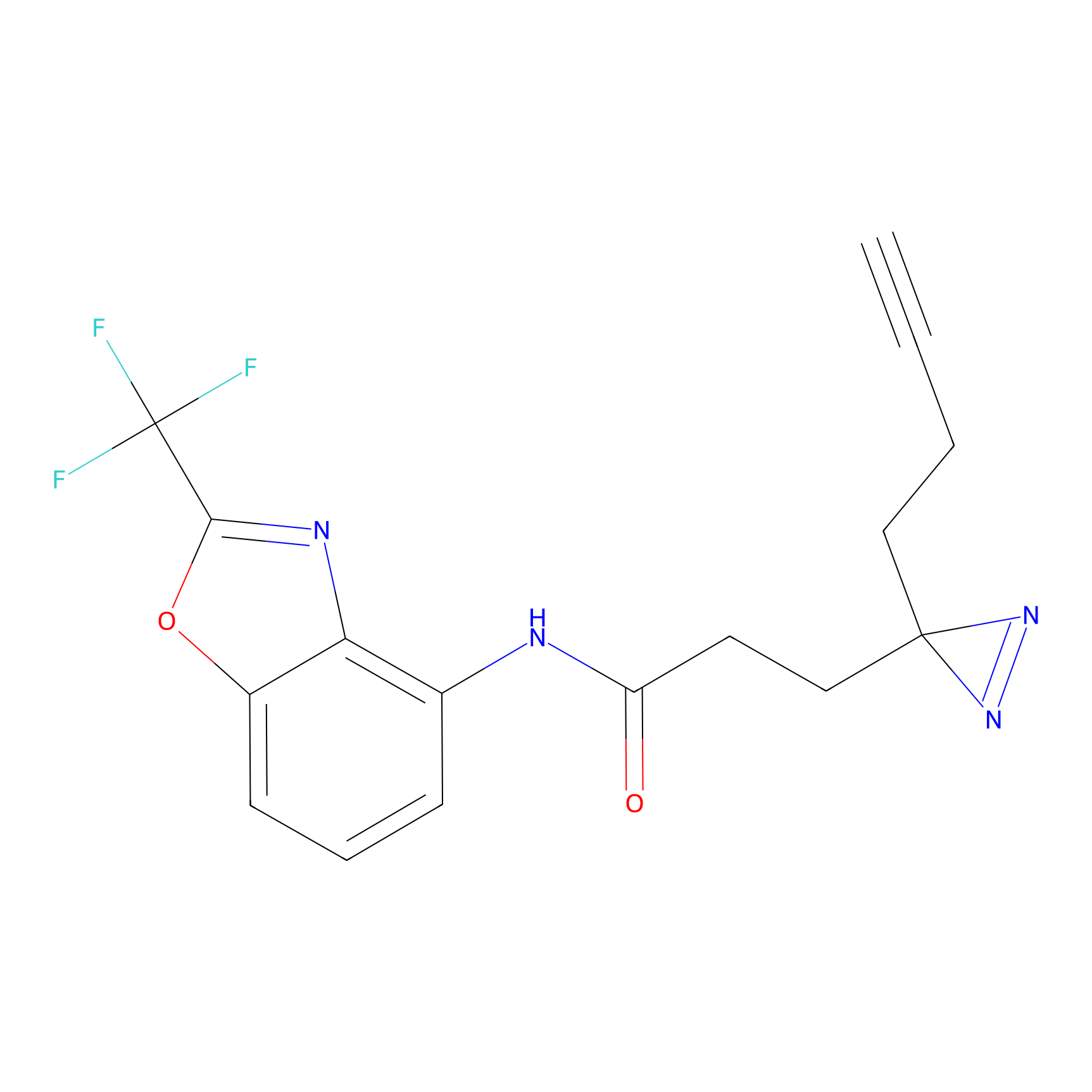
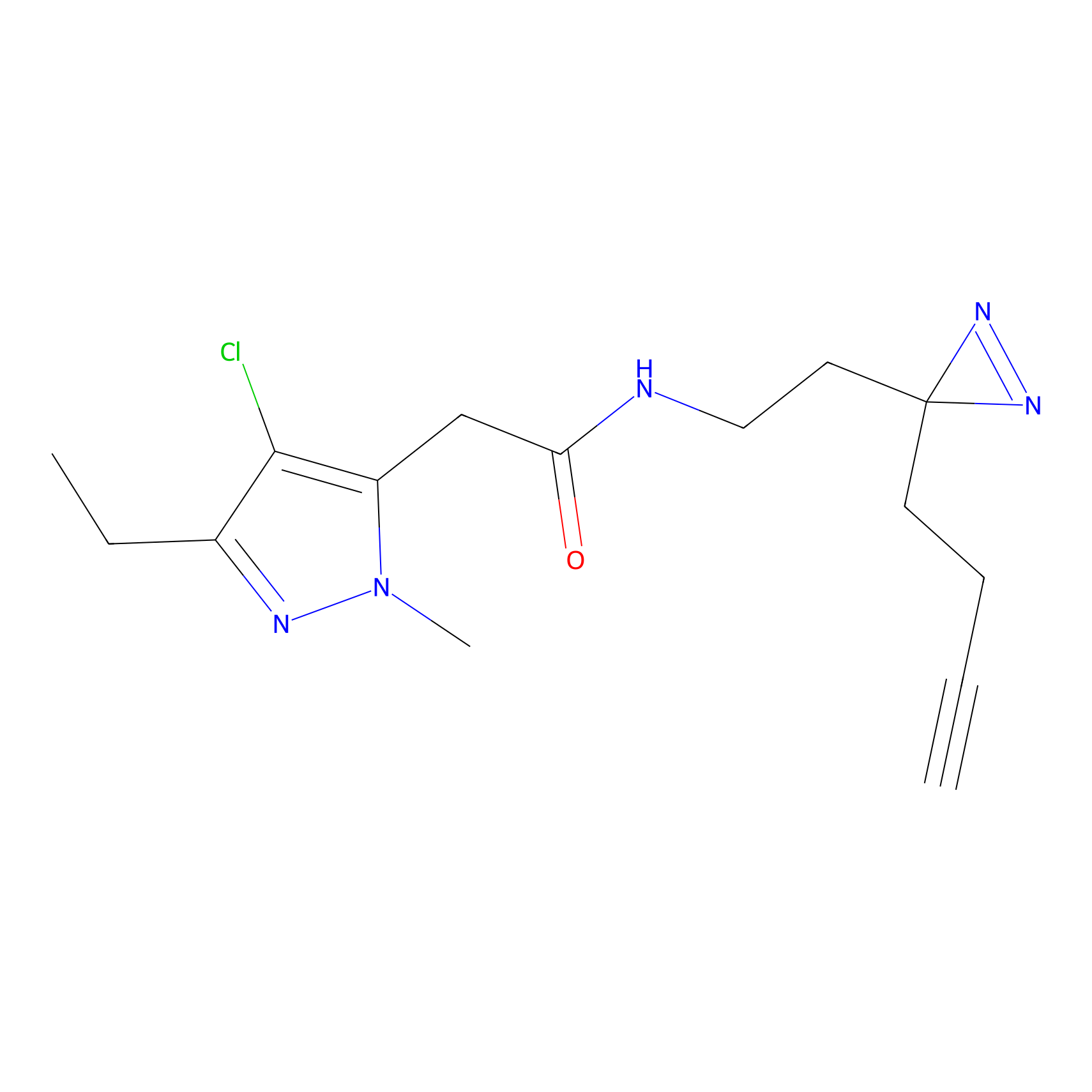
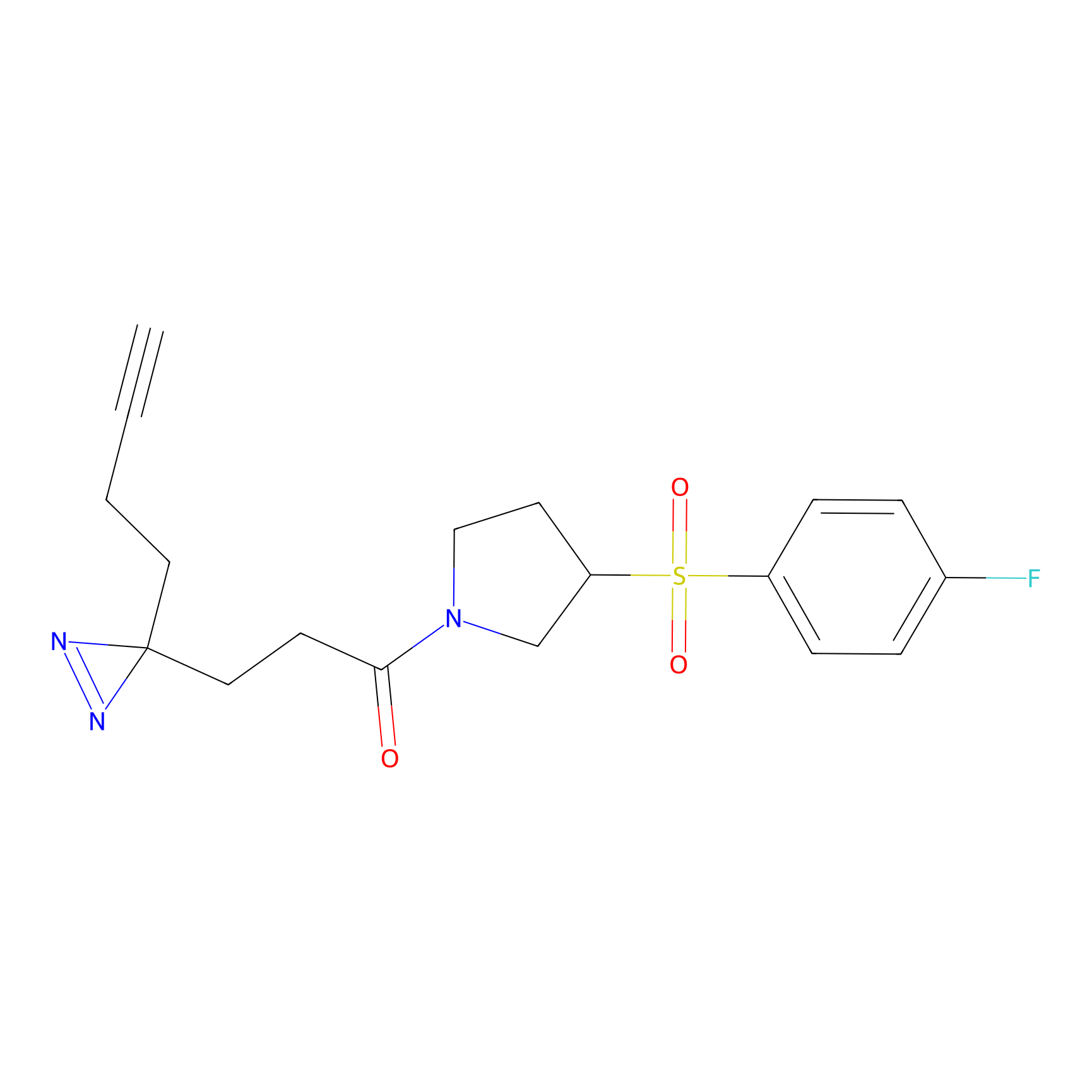
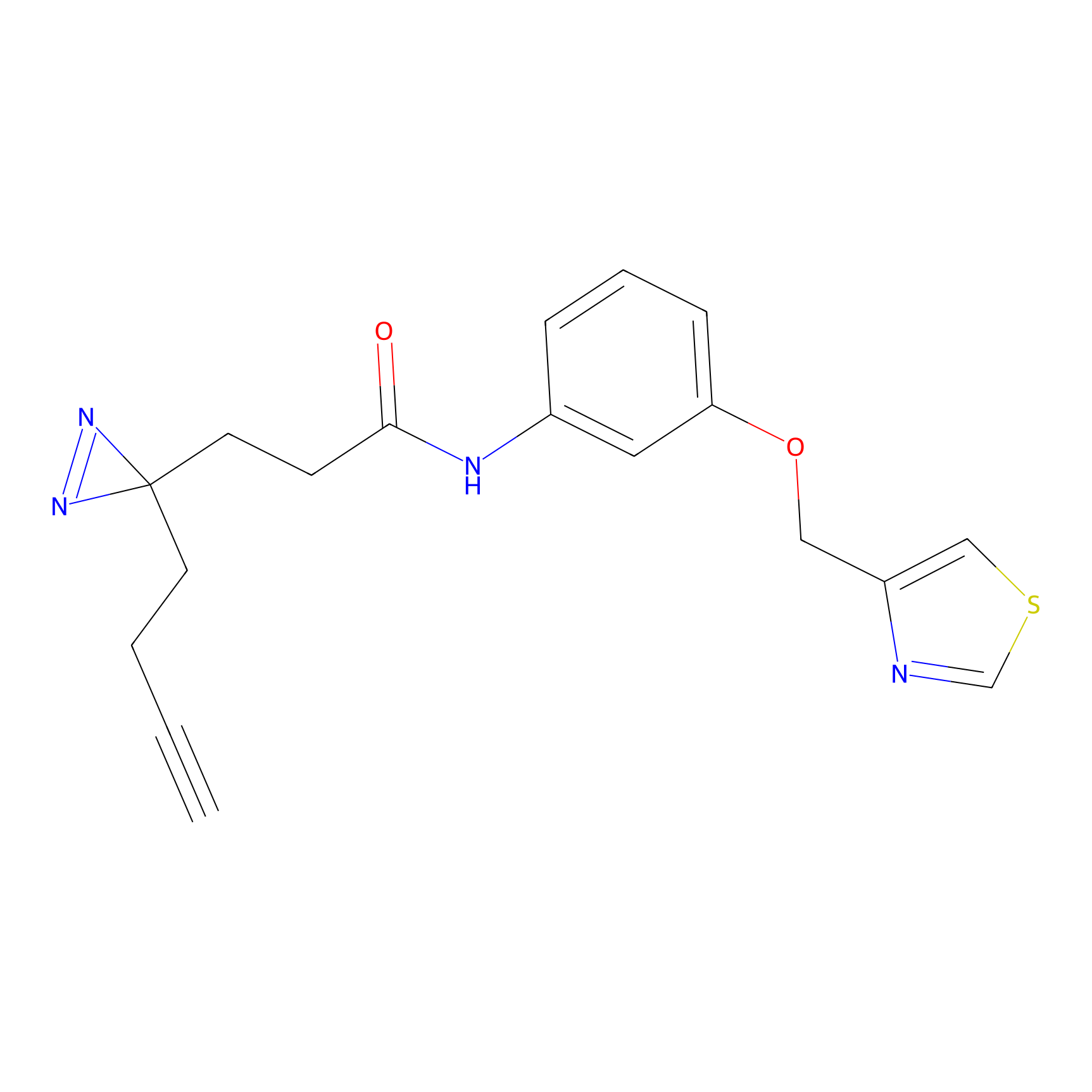
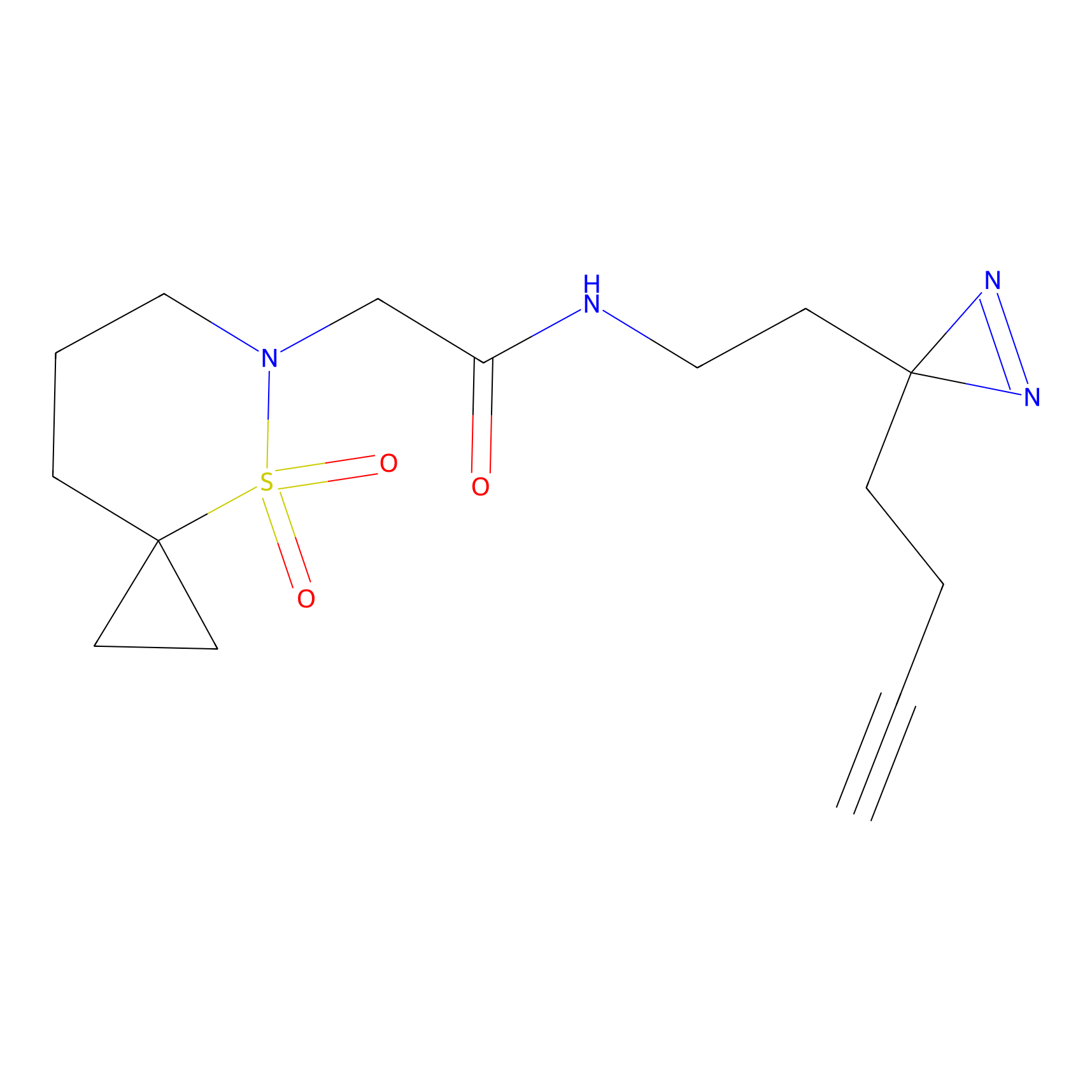
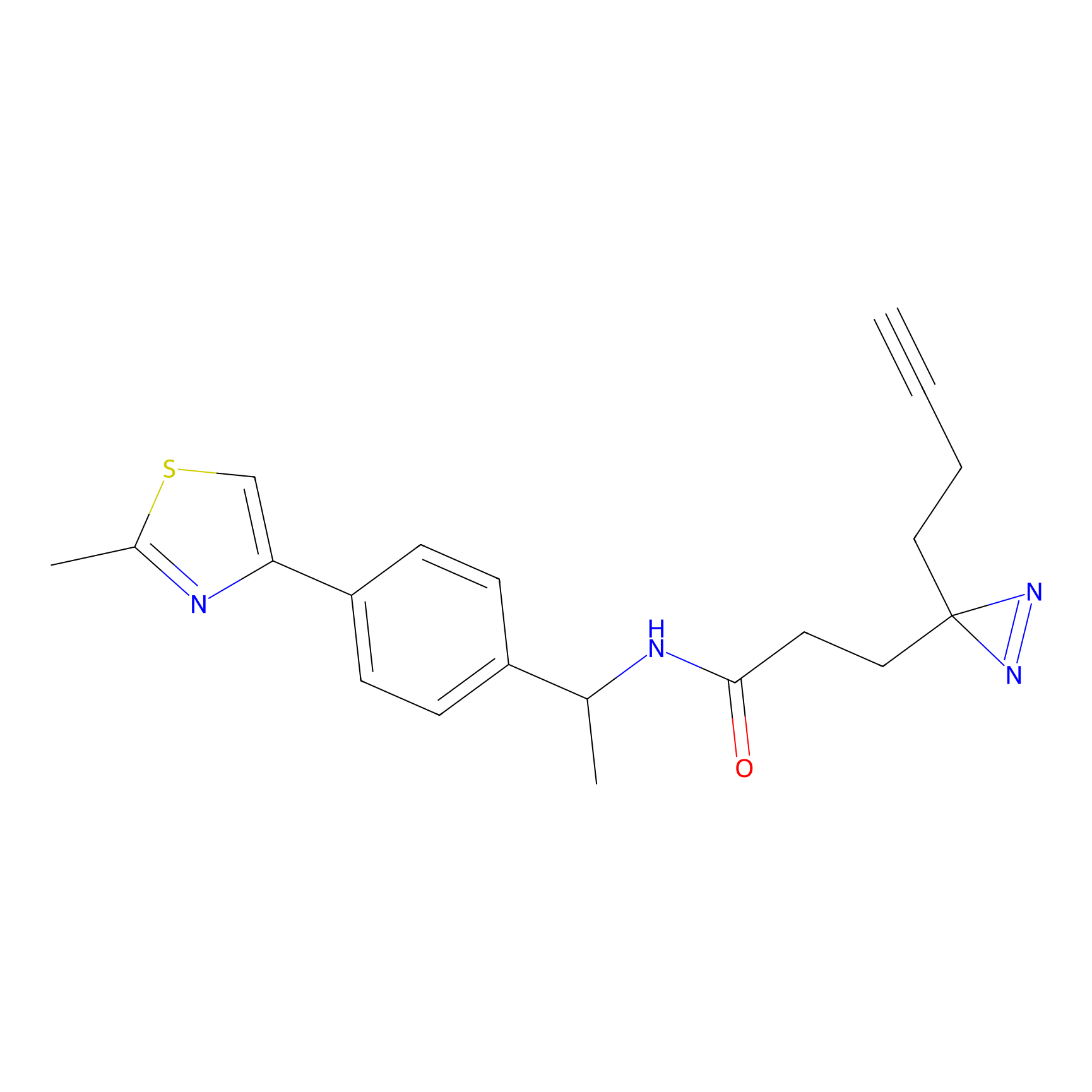
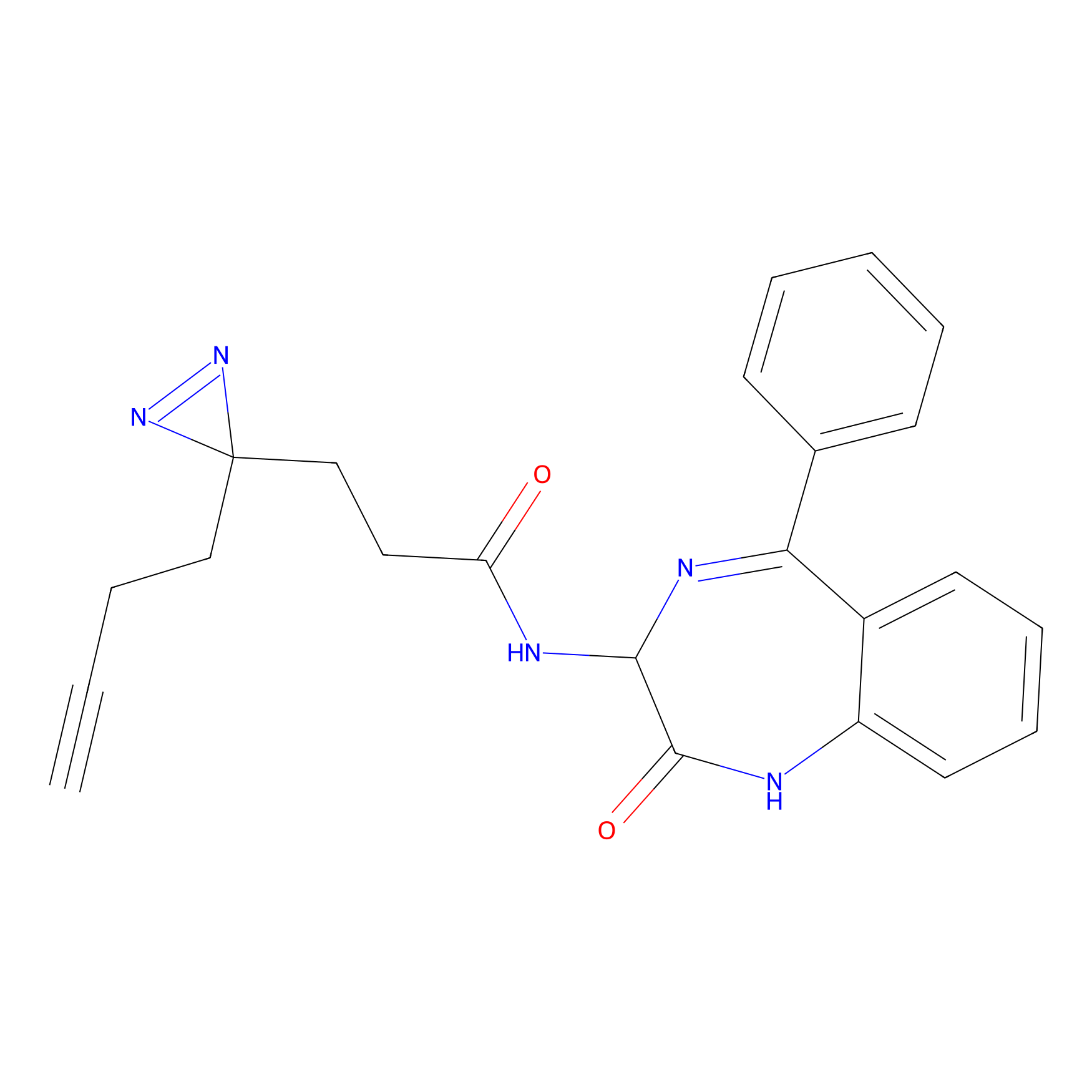
YN-4 Probe Info |
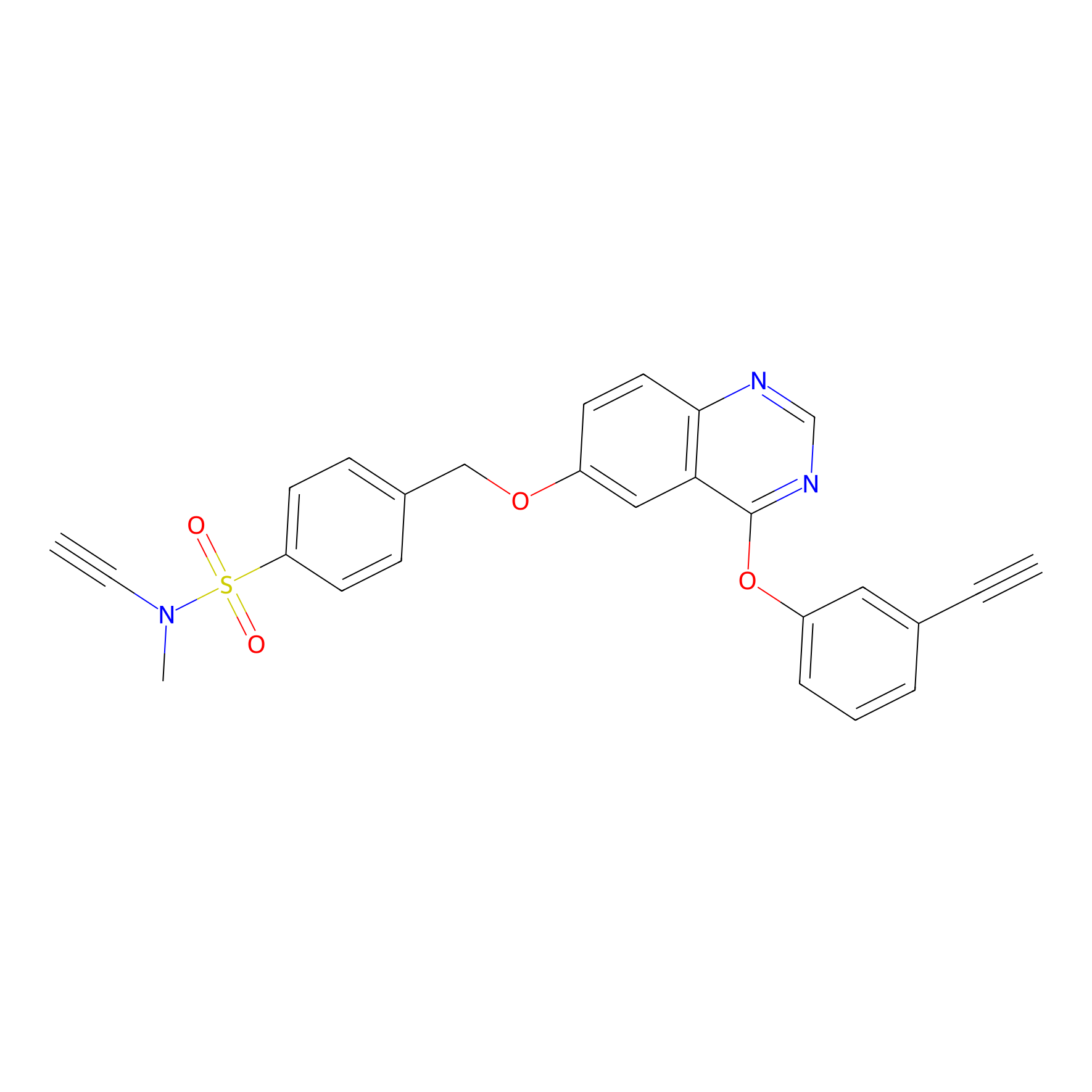 |
100.00 | LDD0445 | [2] | |
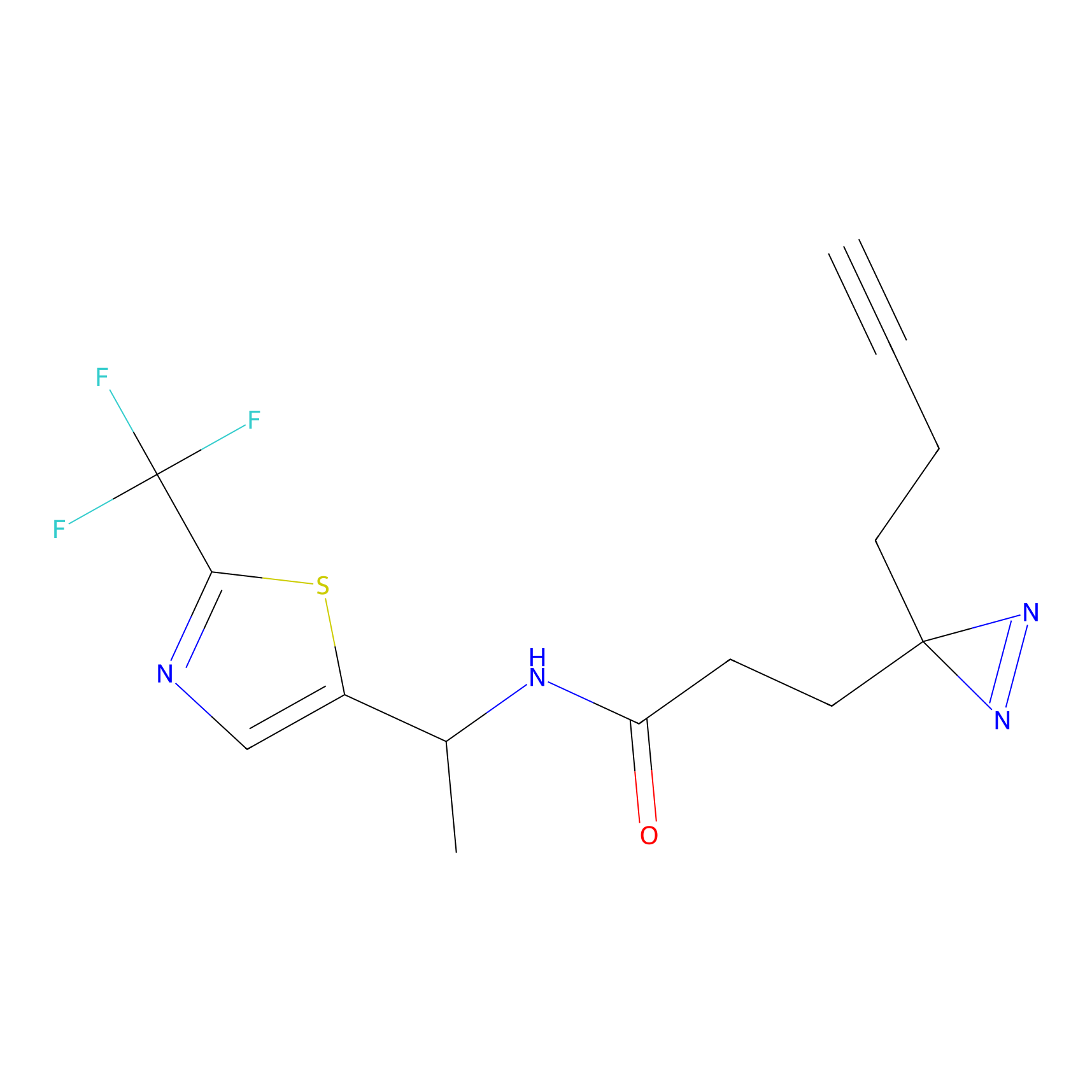
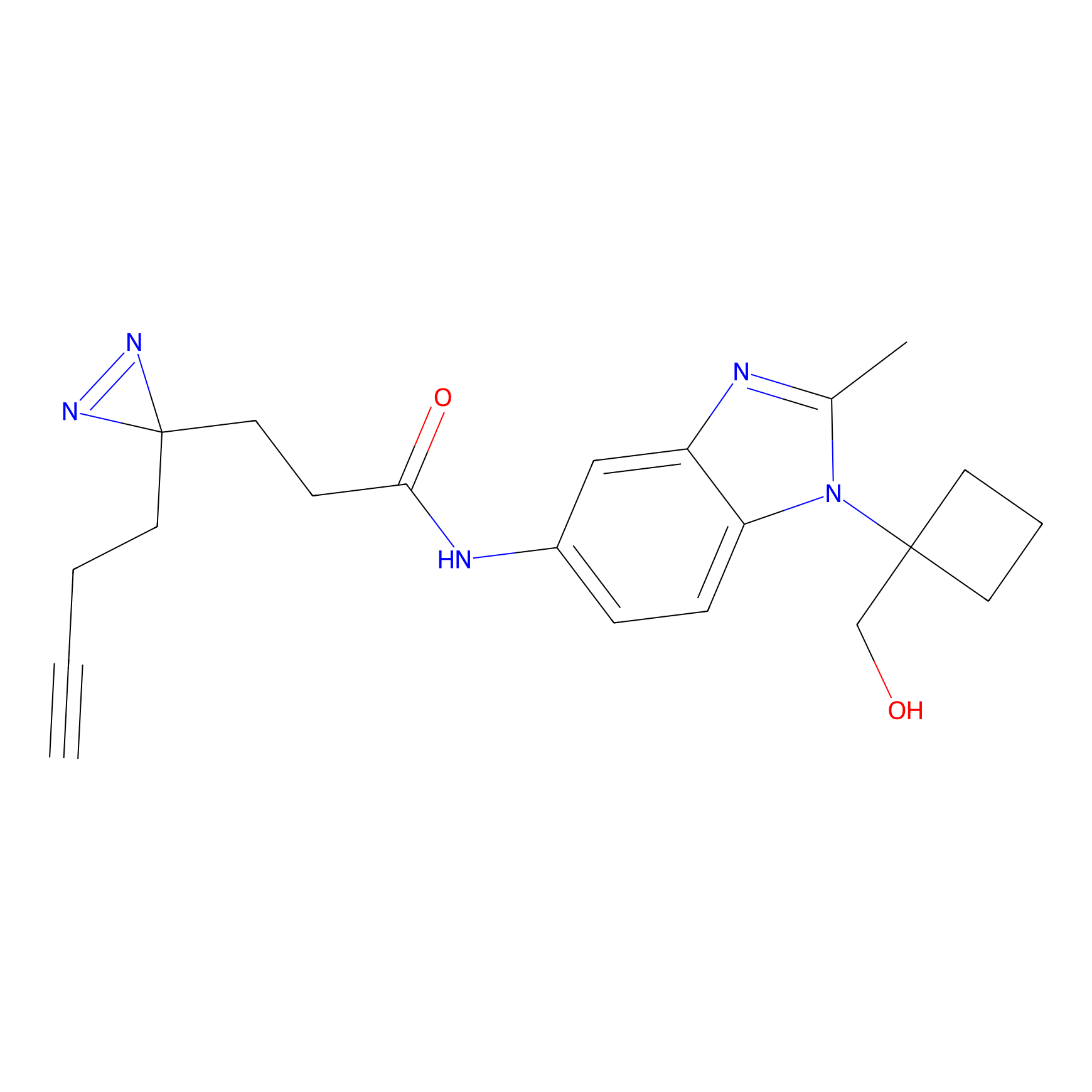
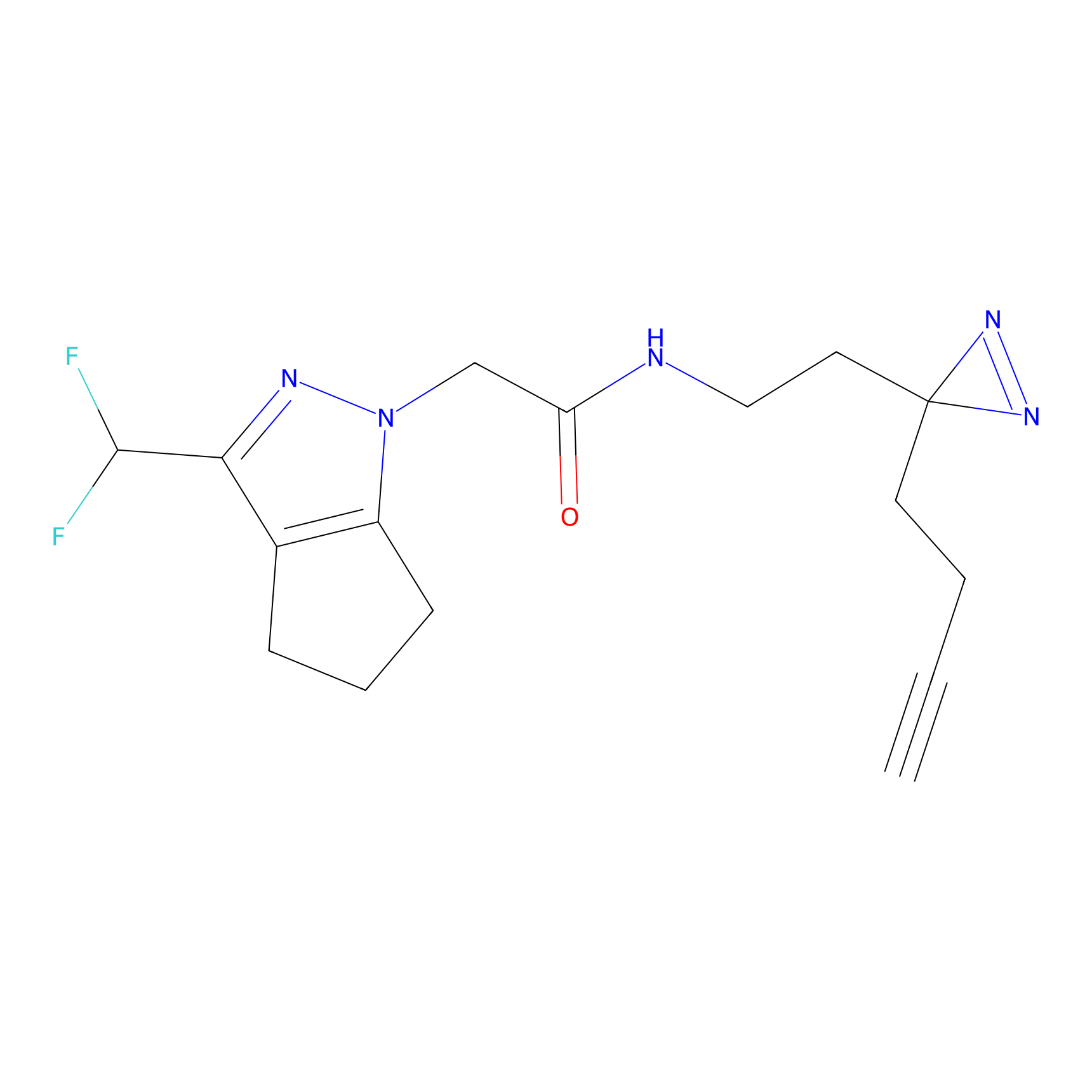
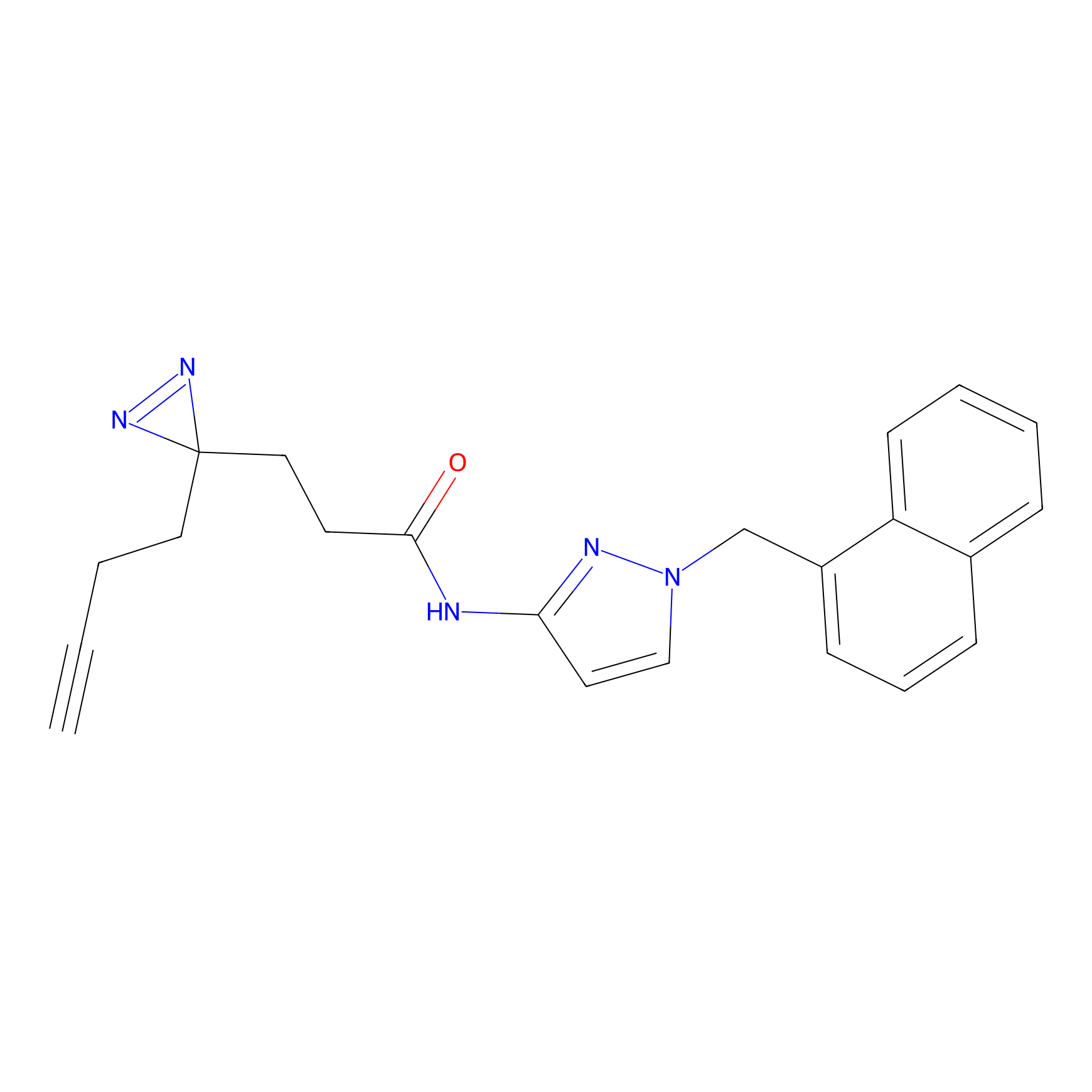
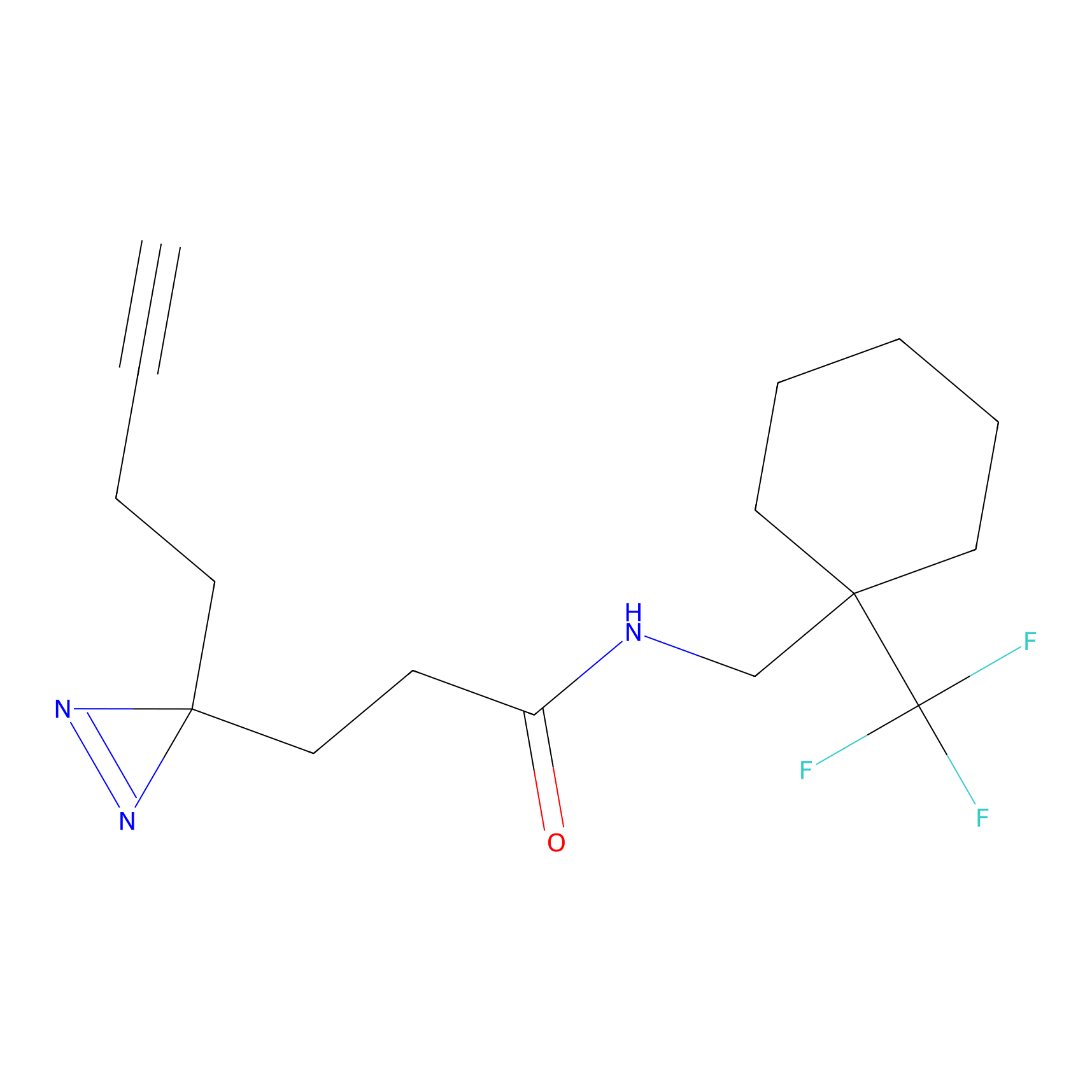
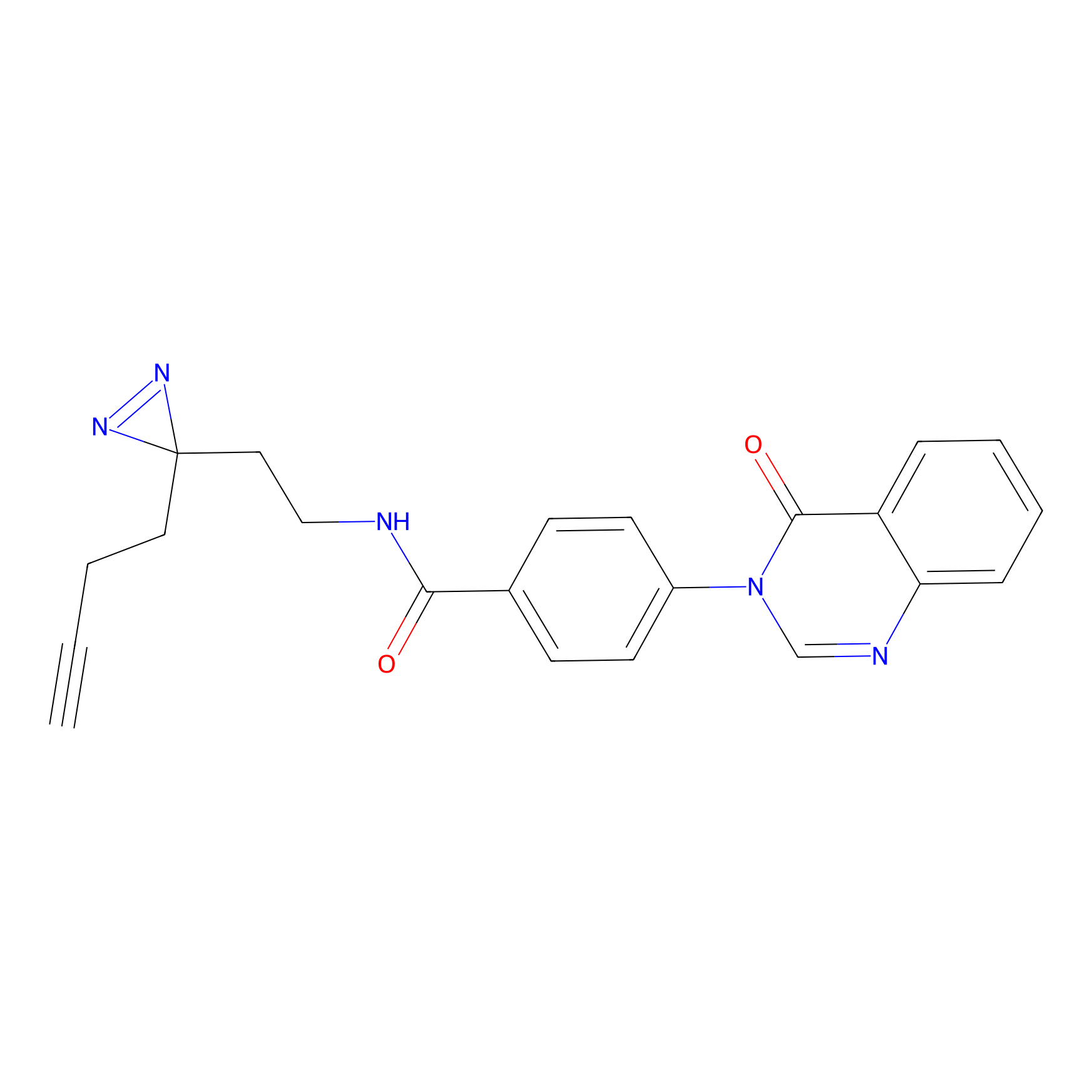
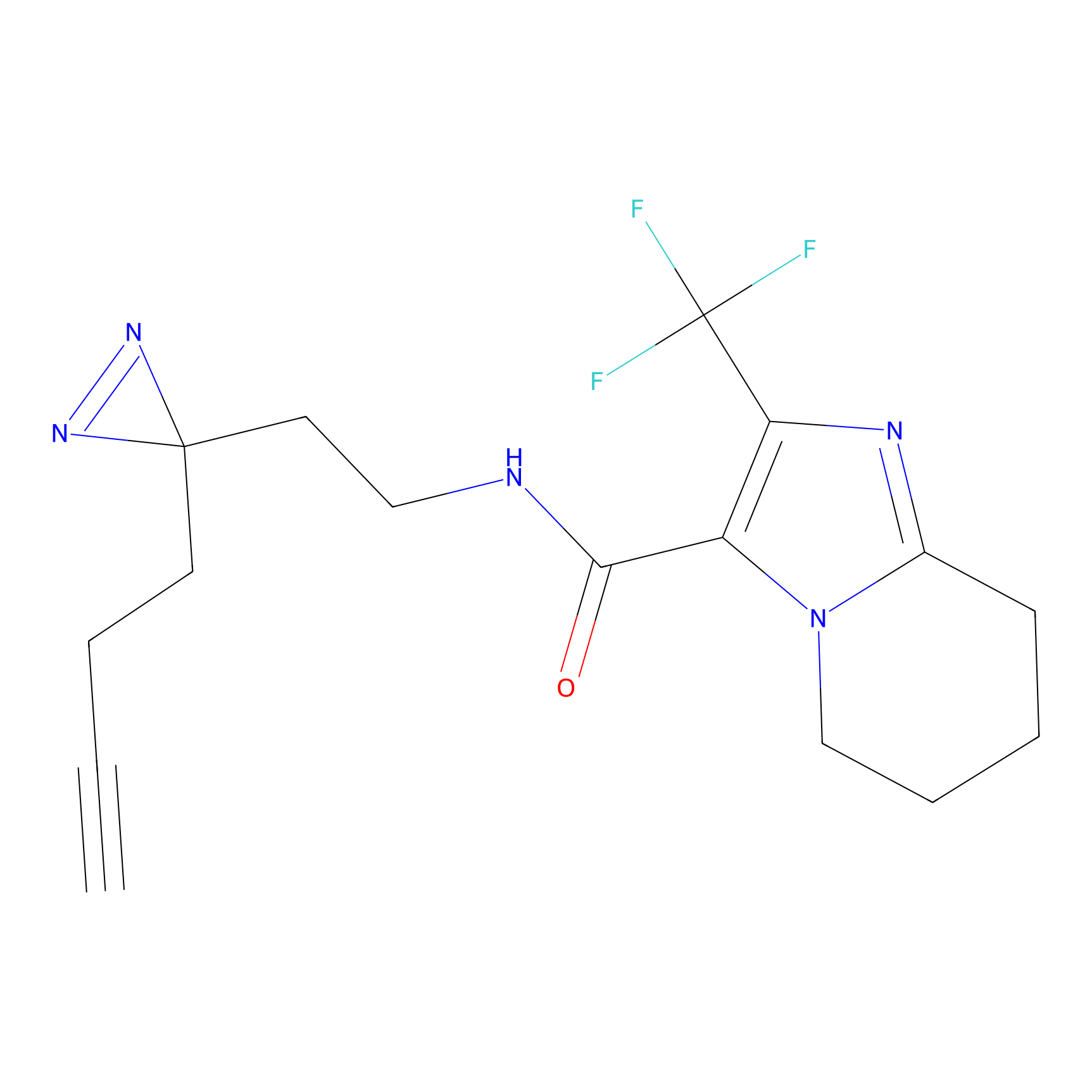
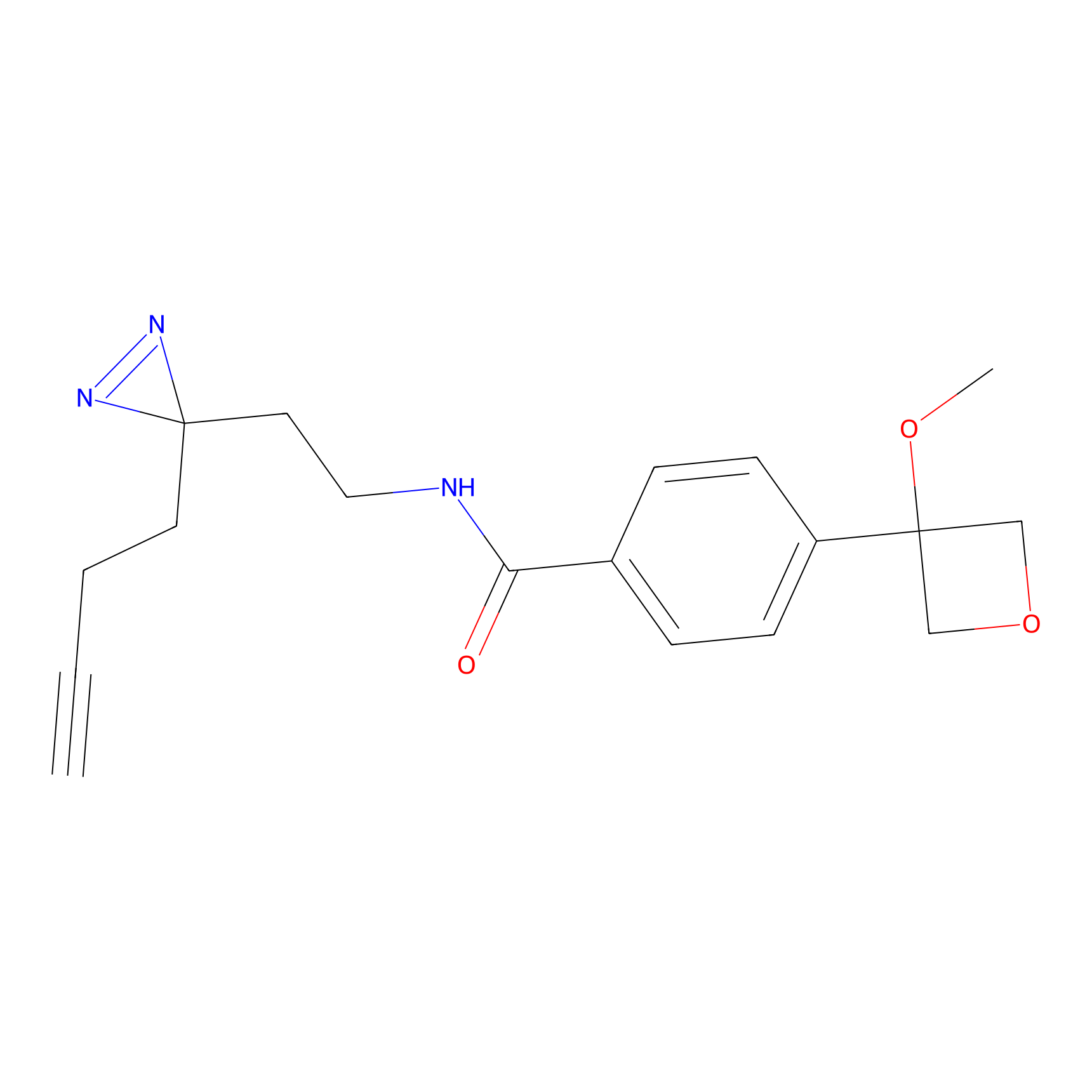
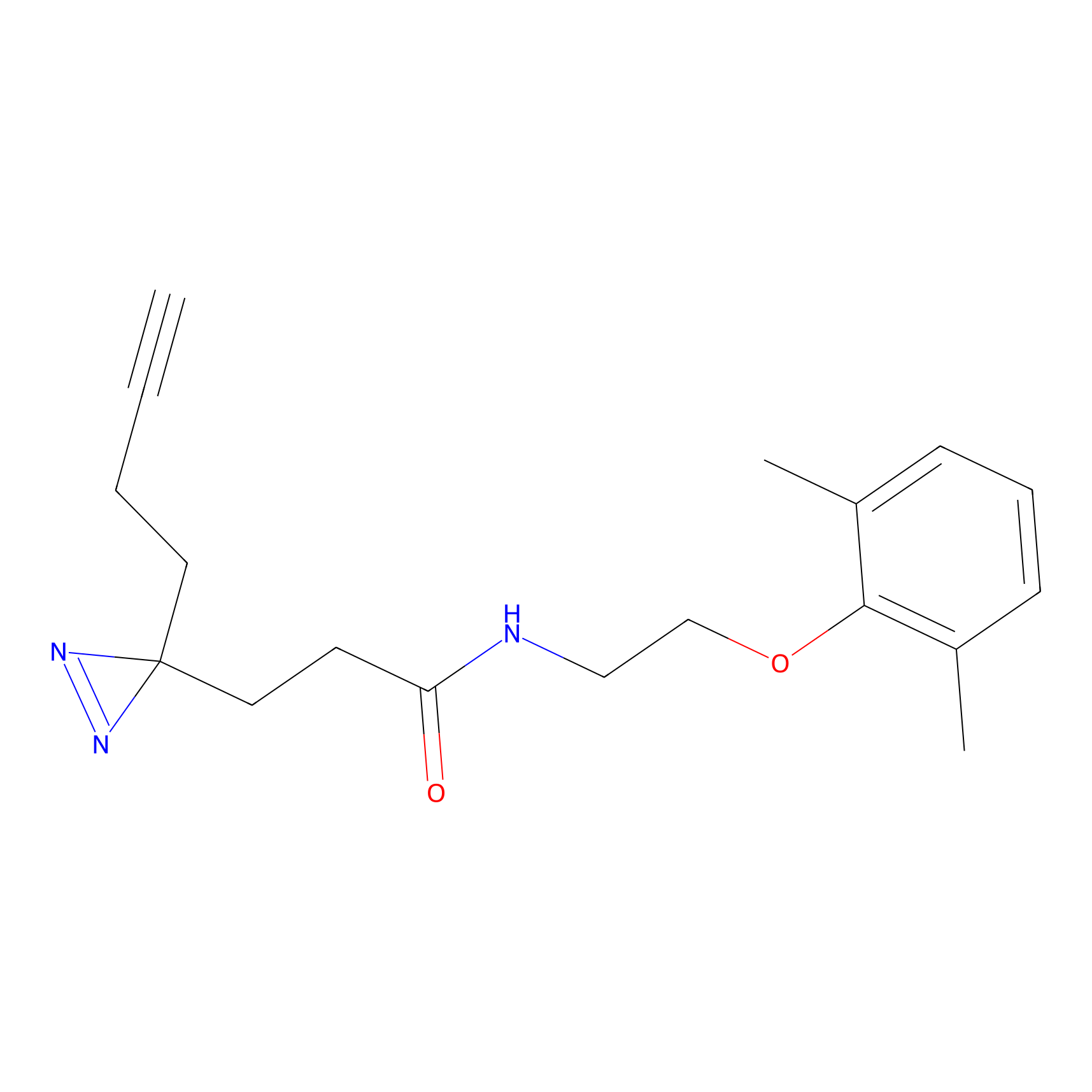
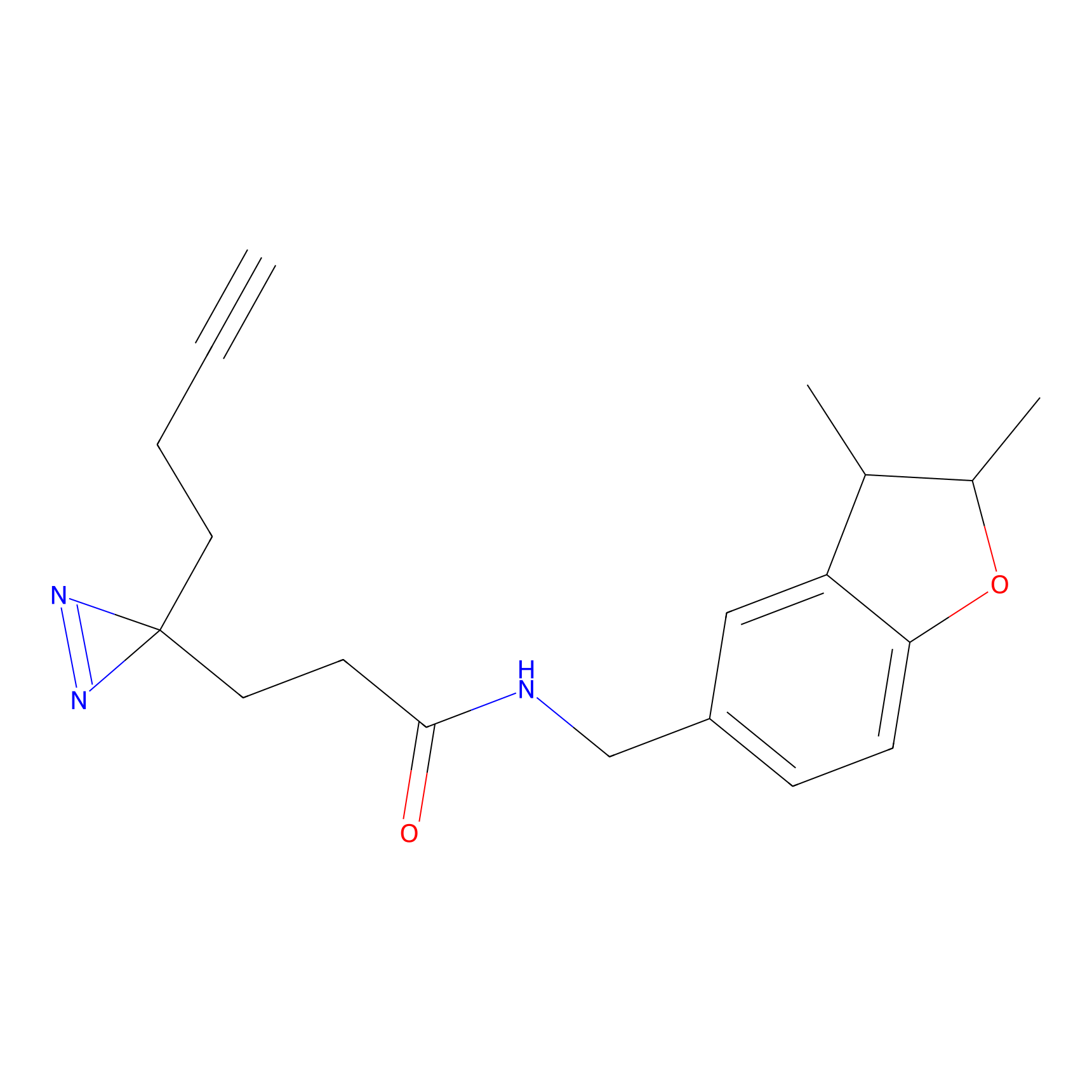
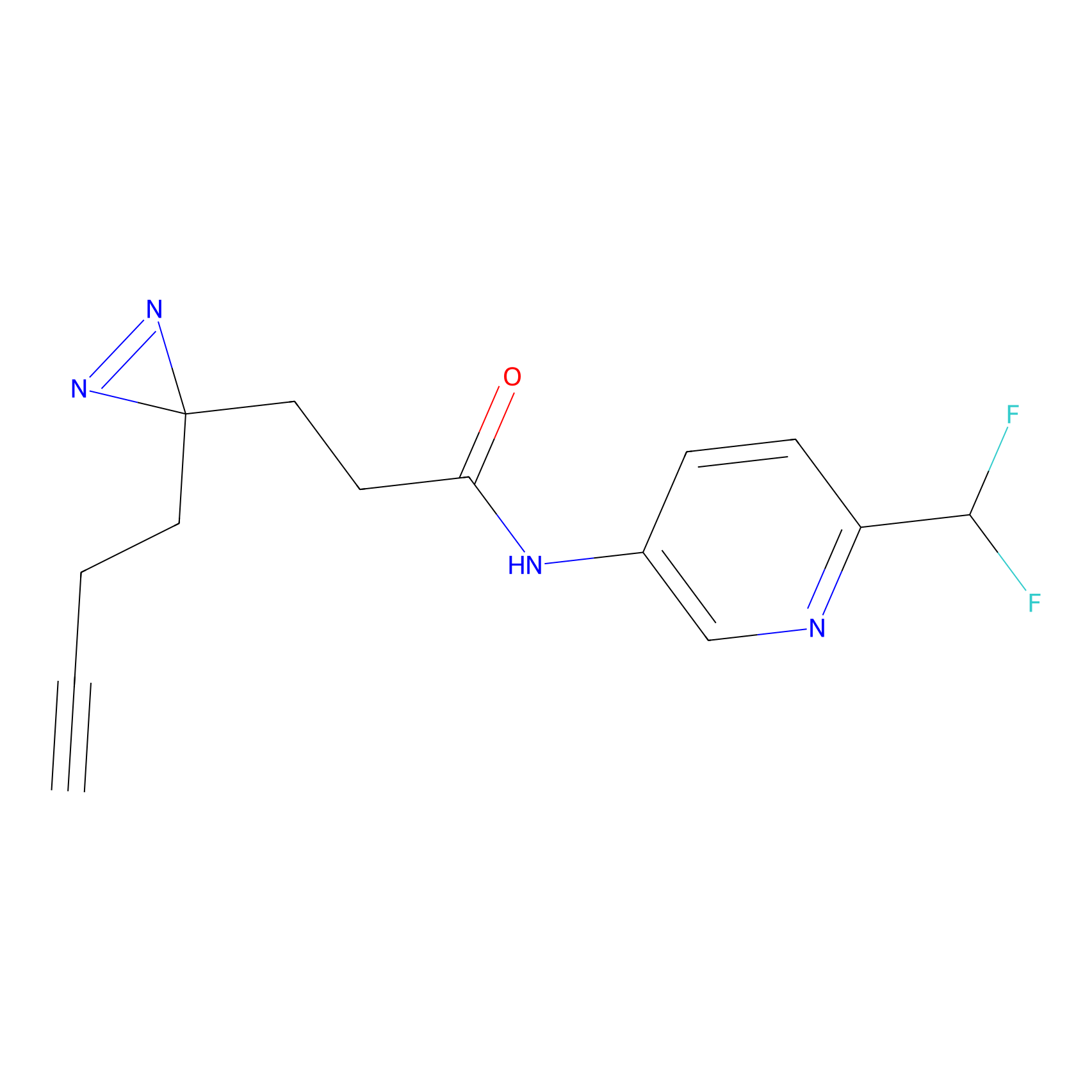
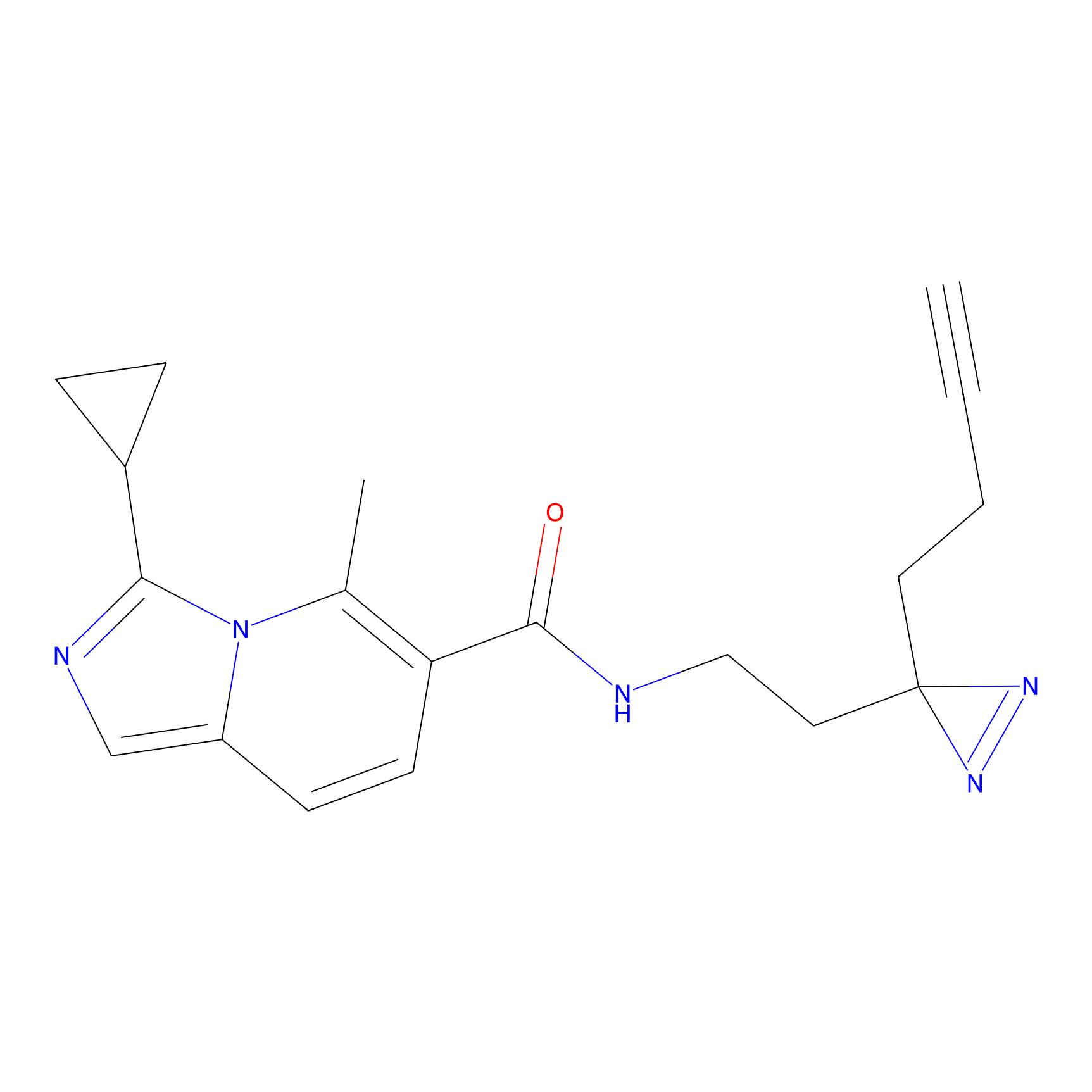
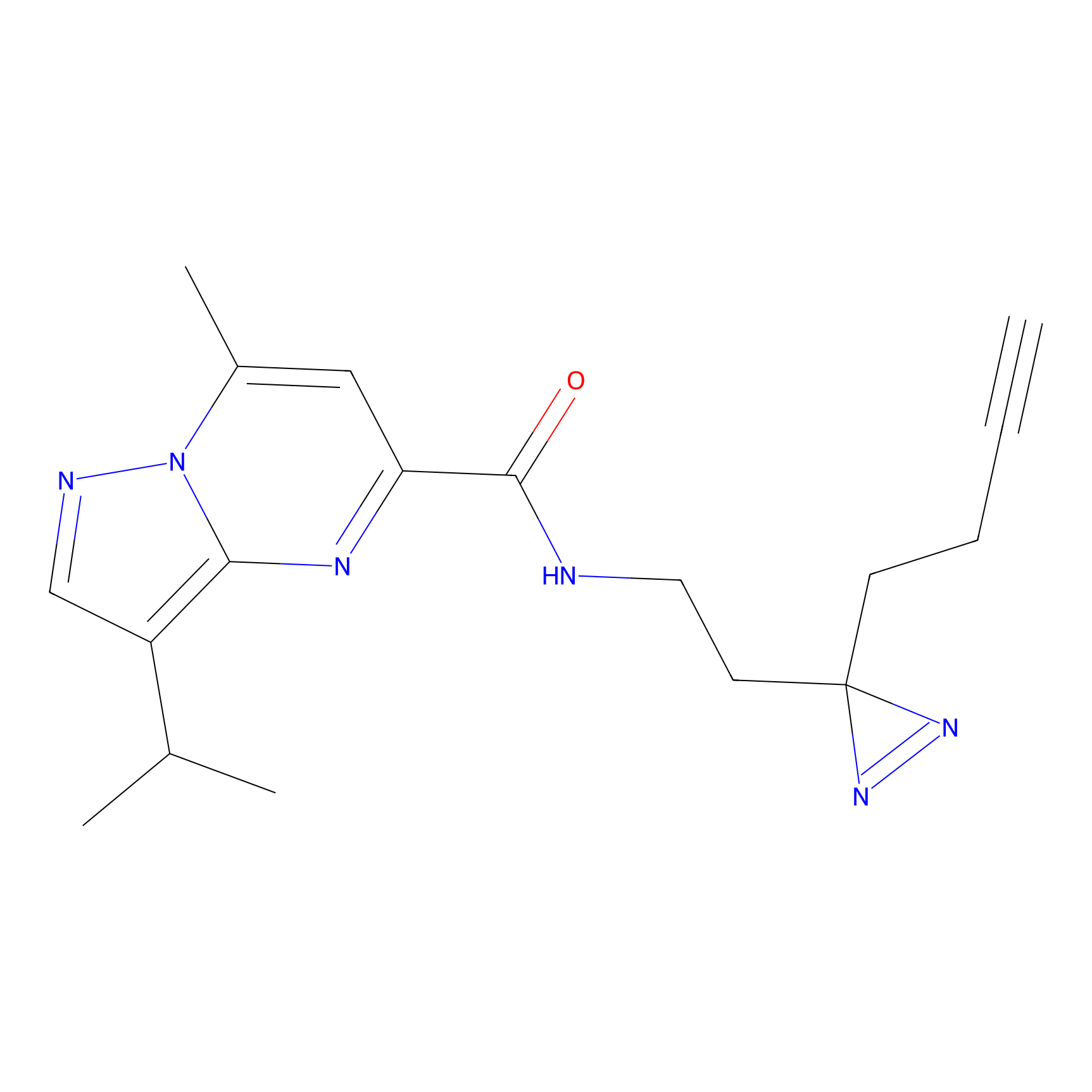
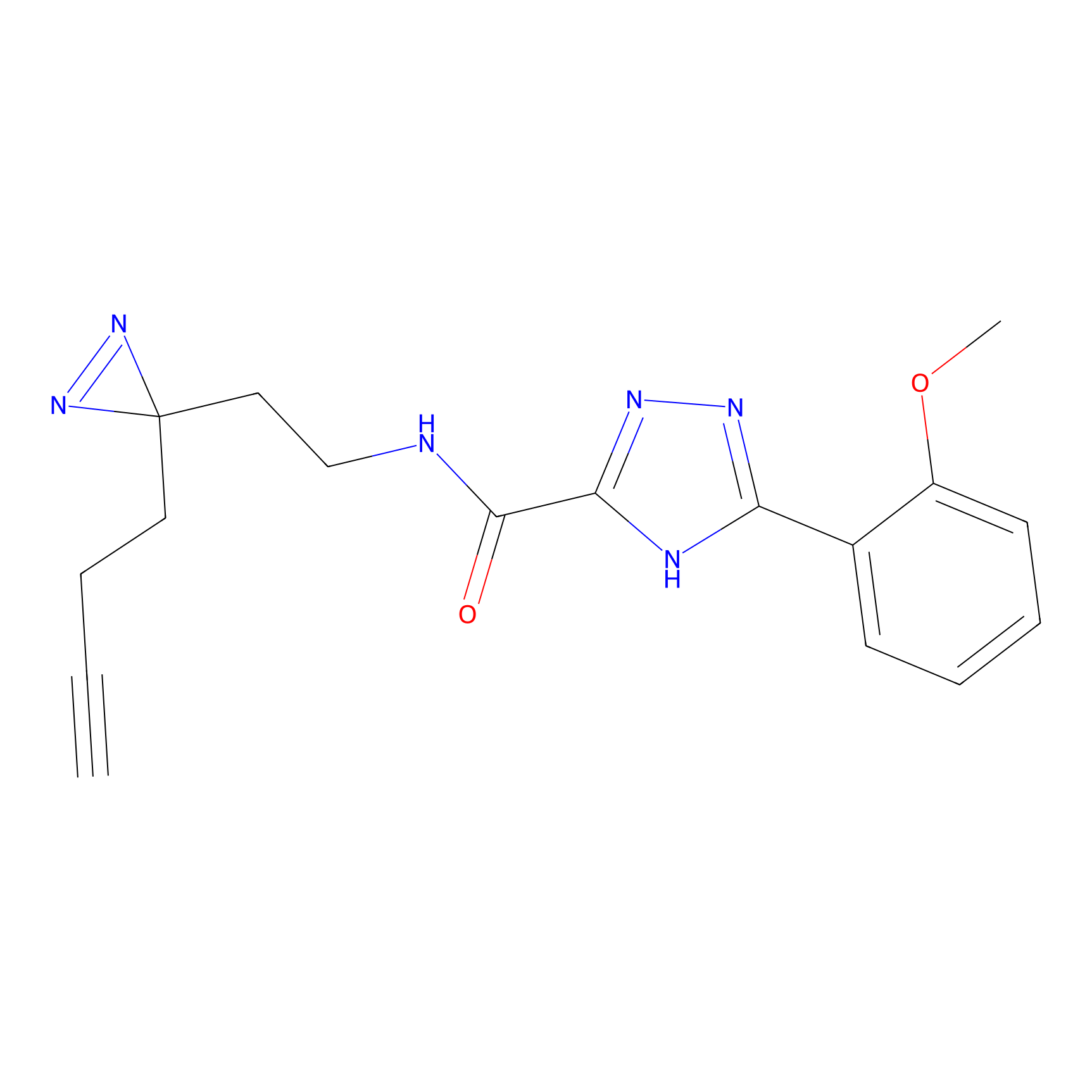
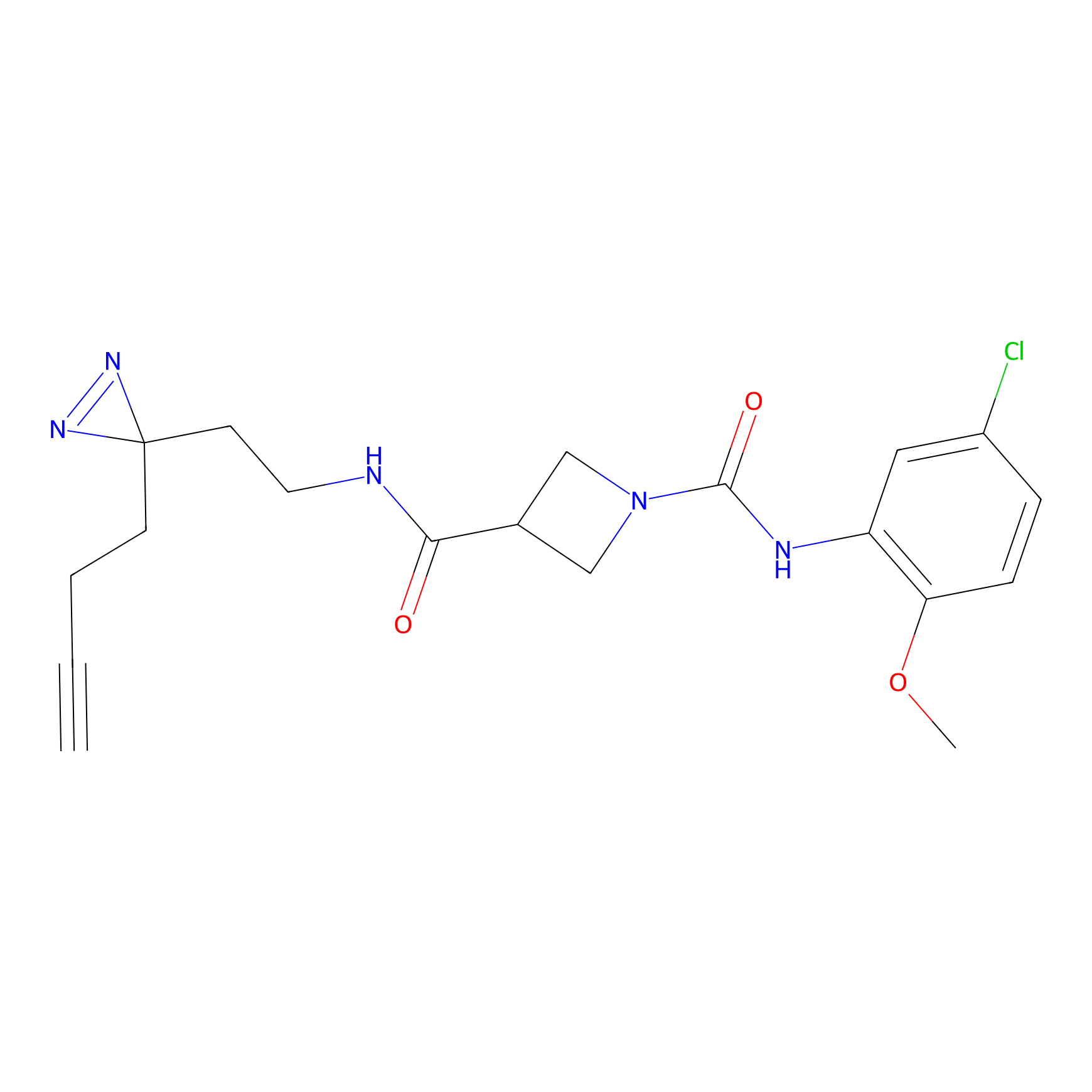
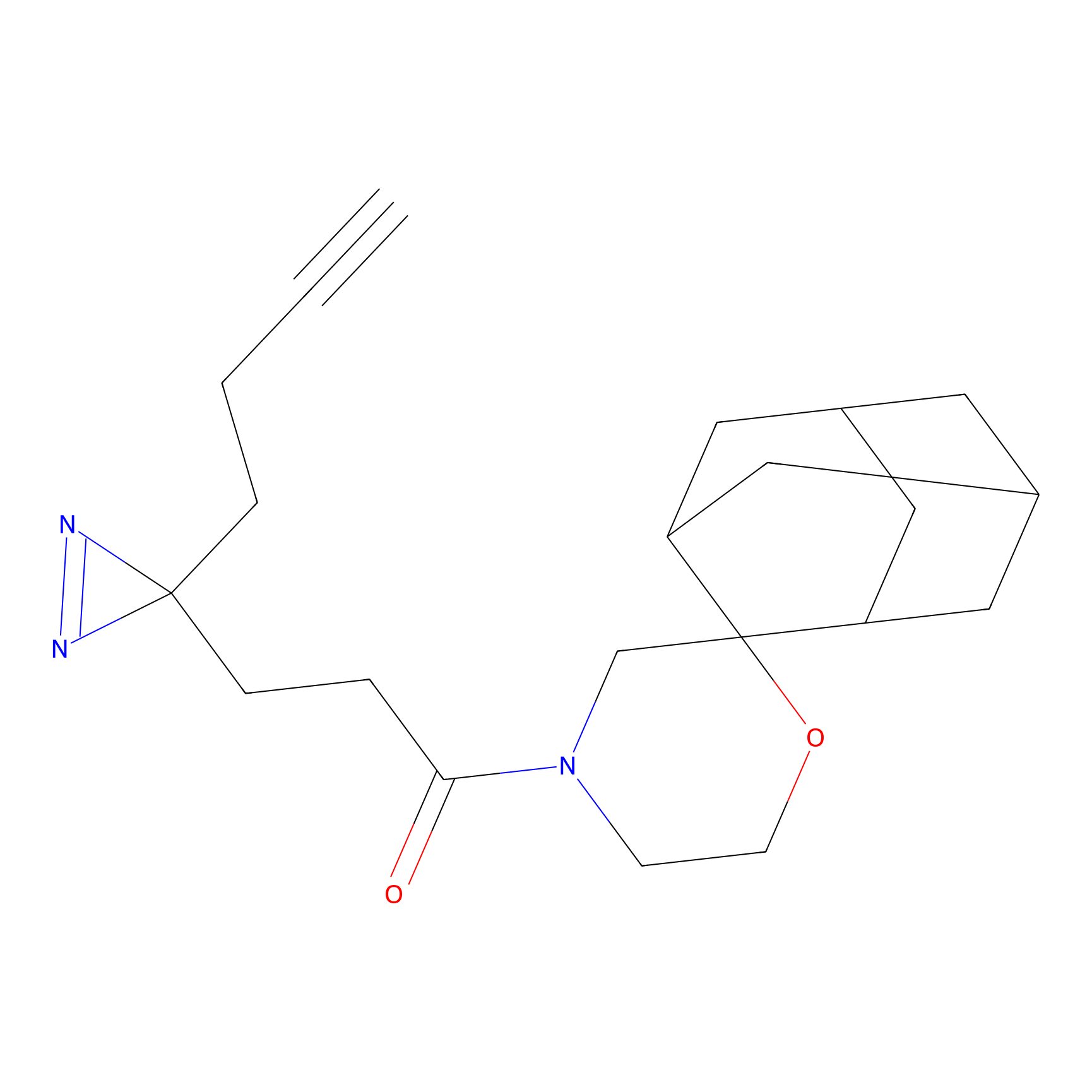
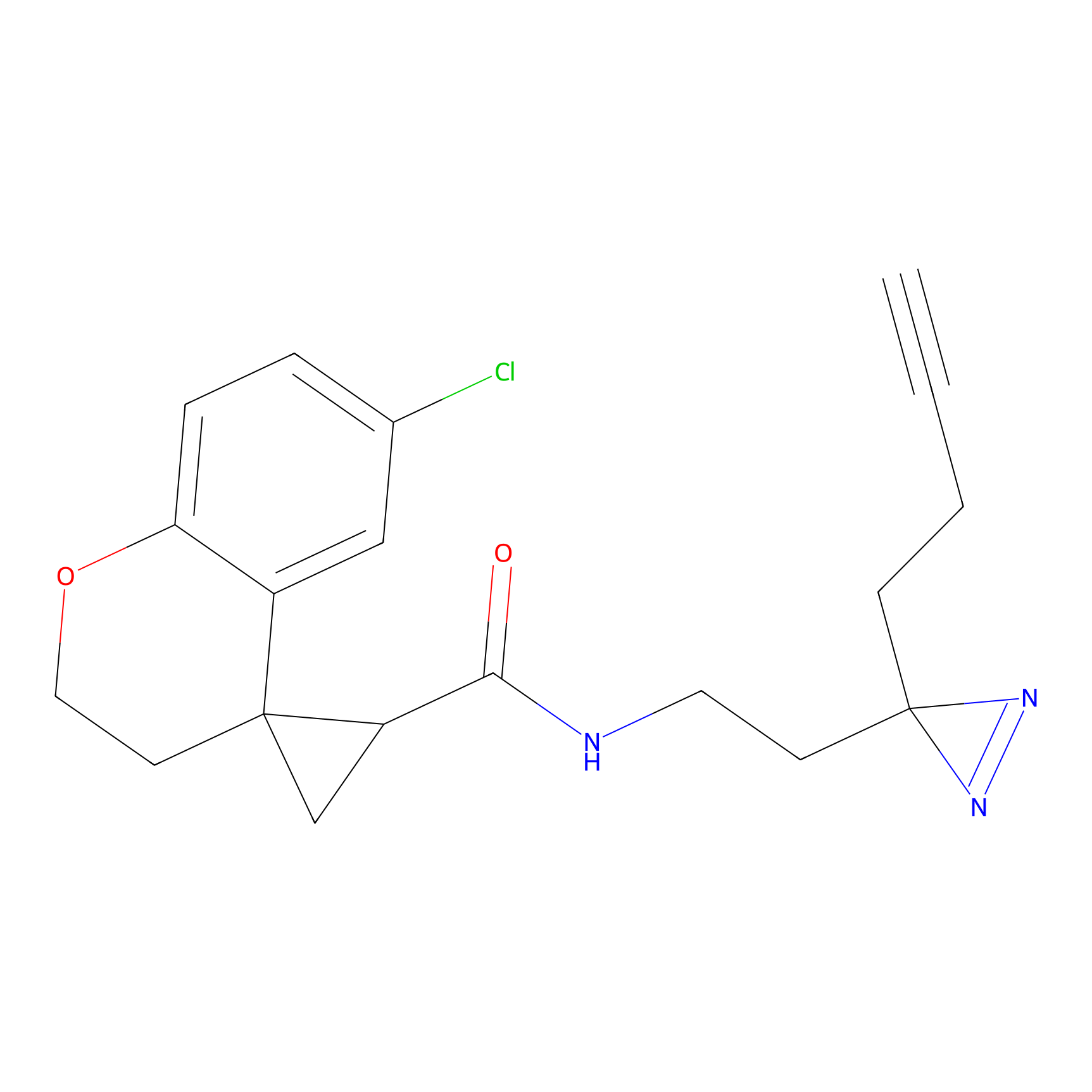
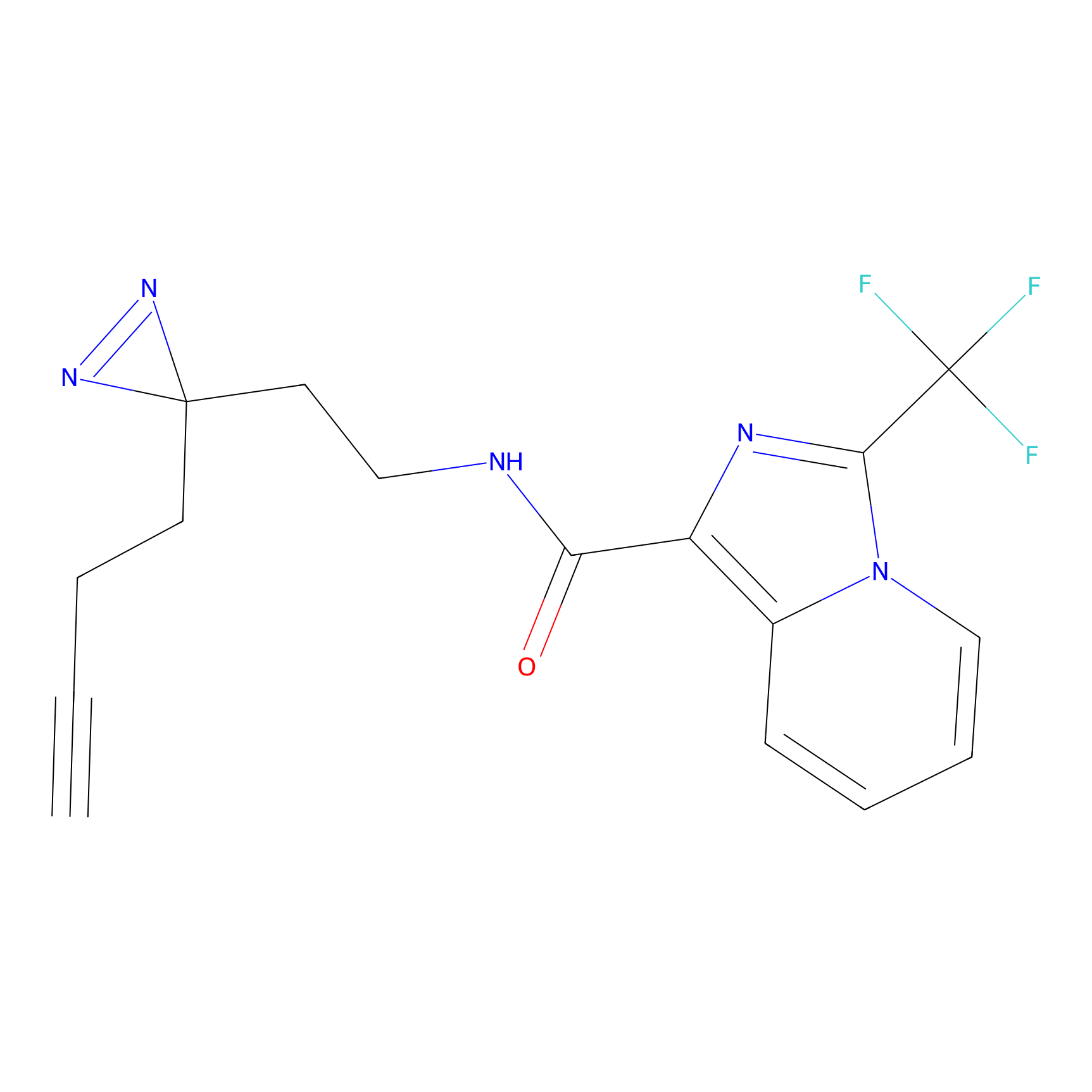
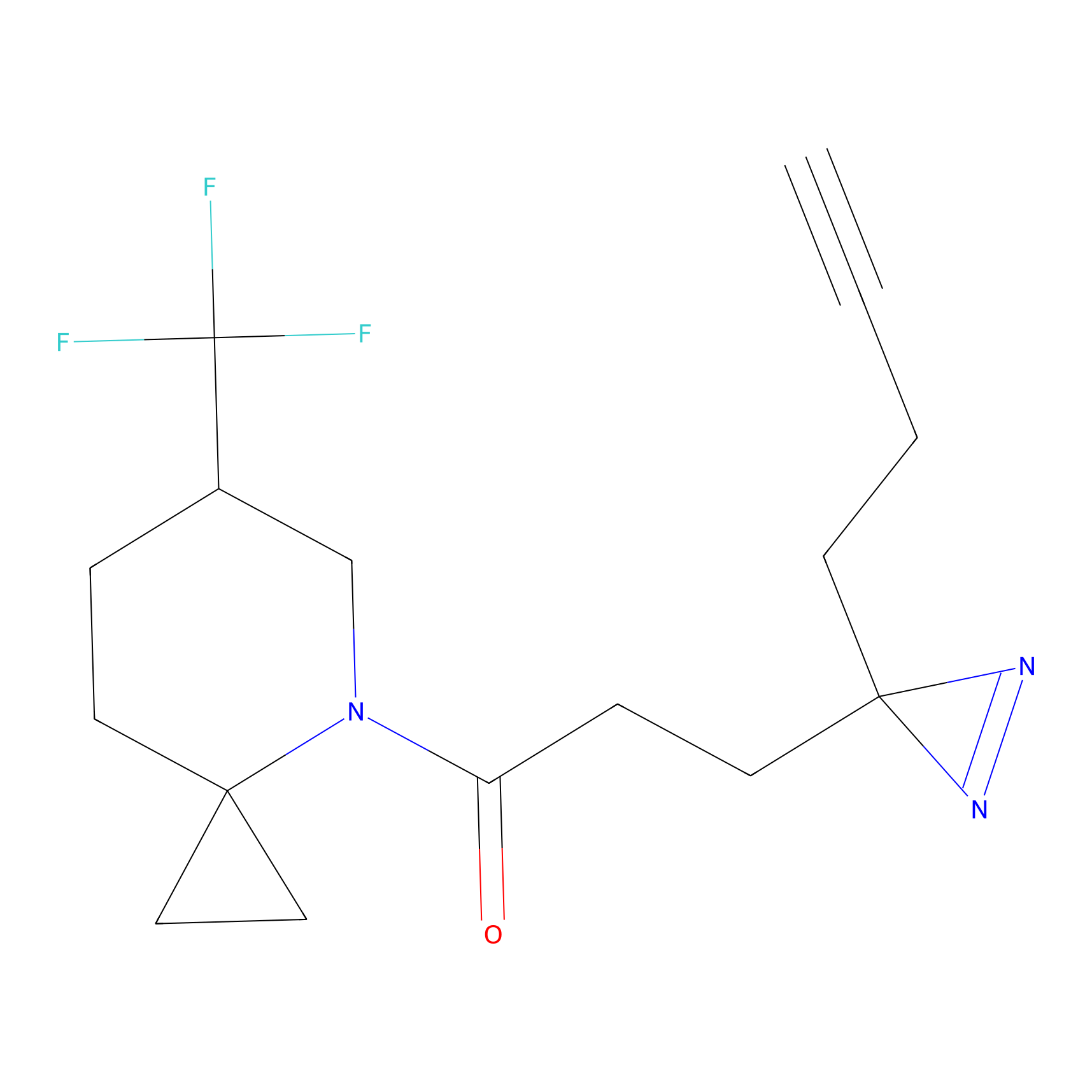
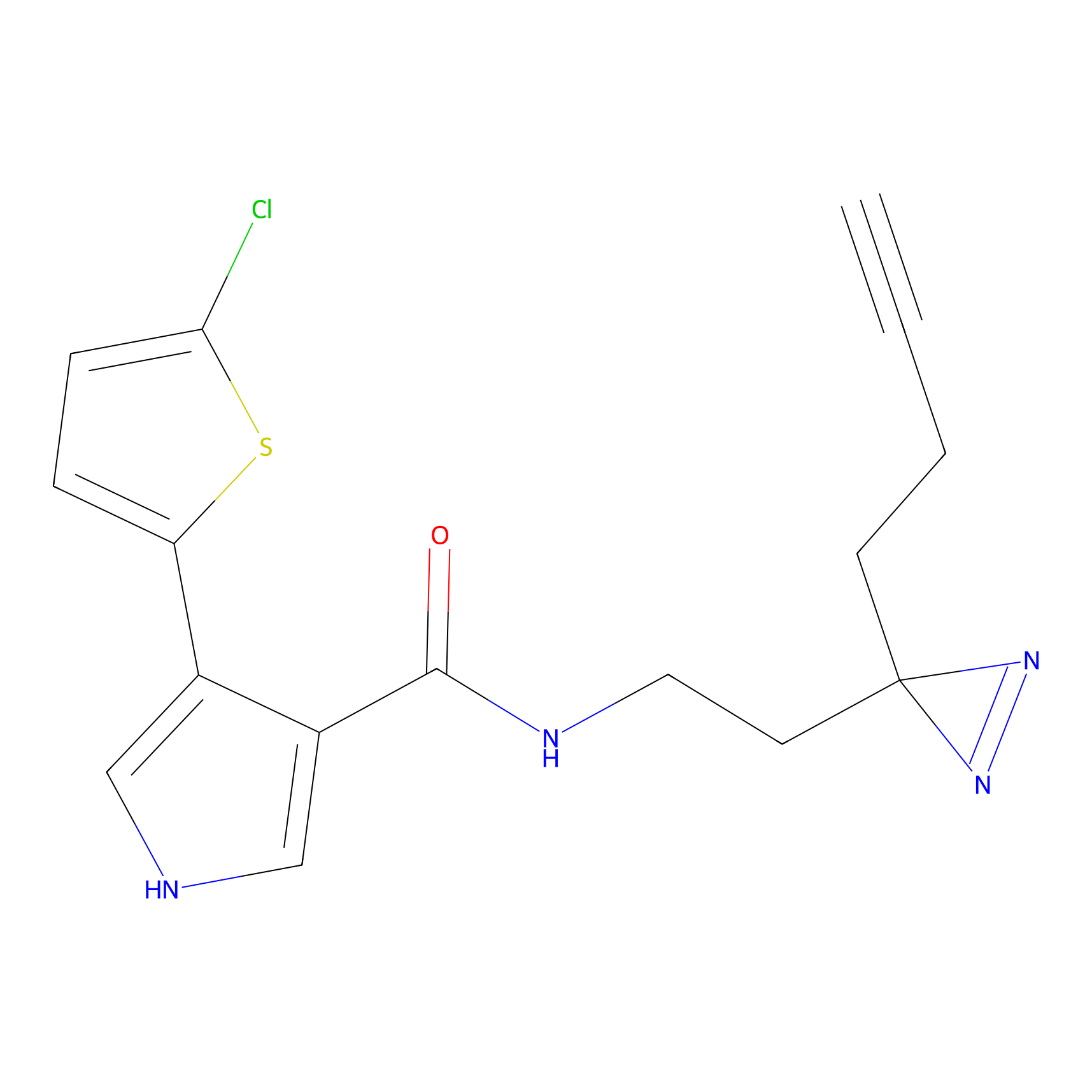
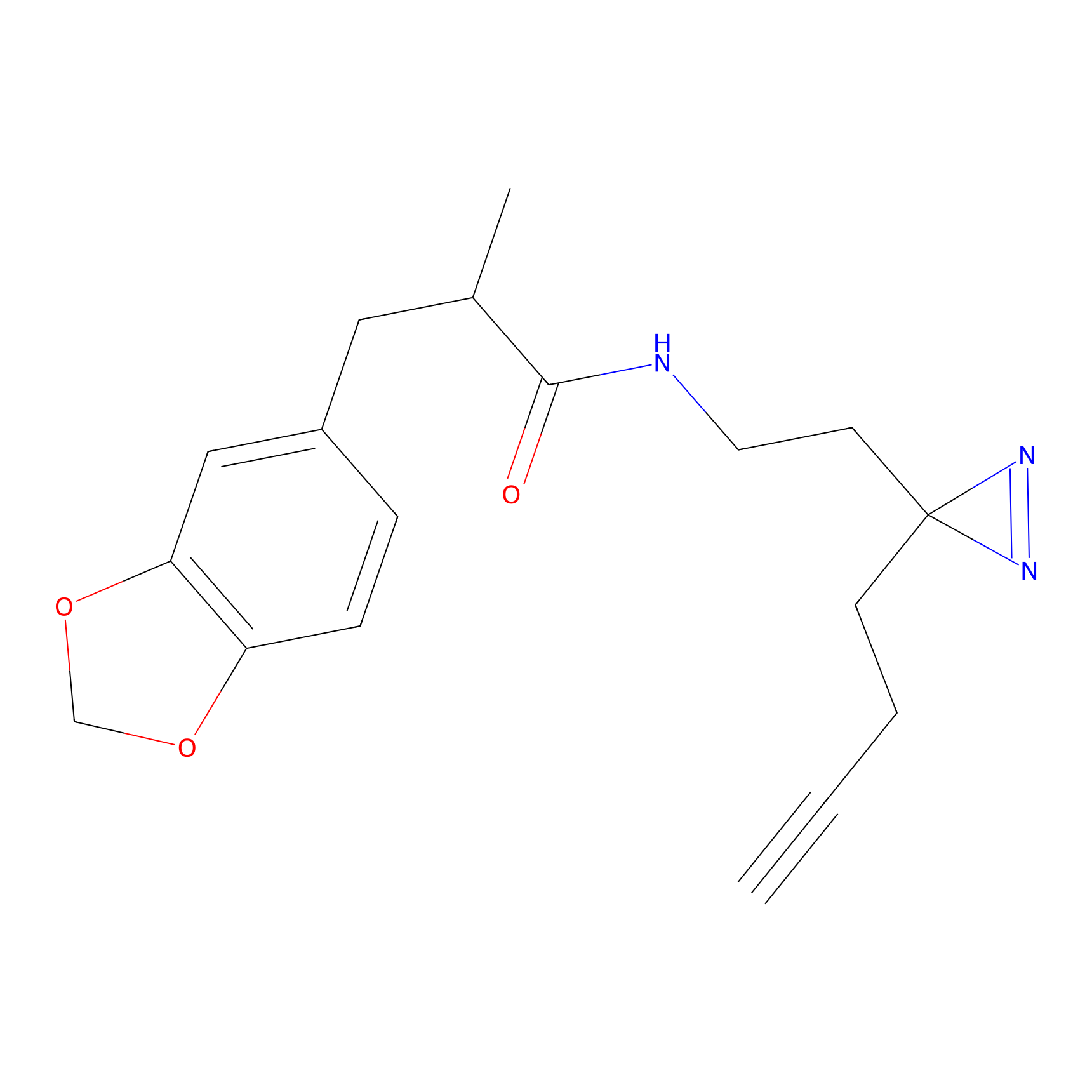
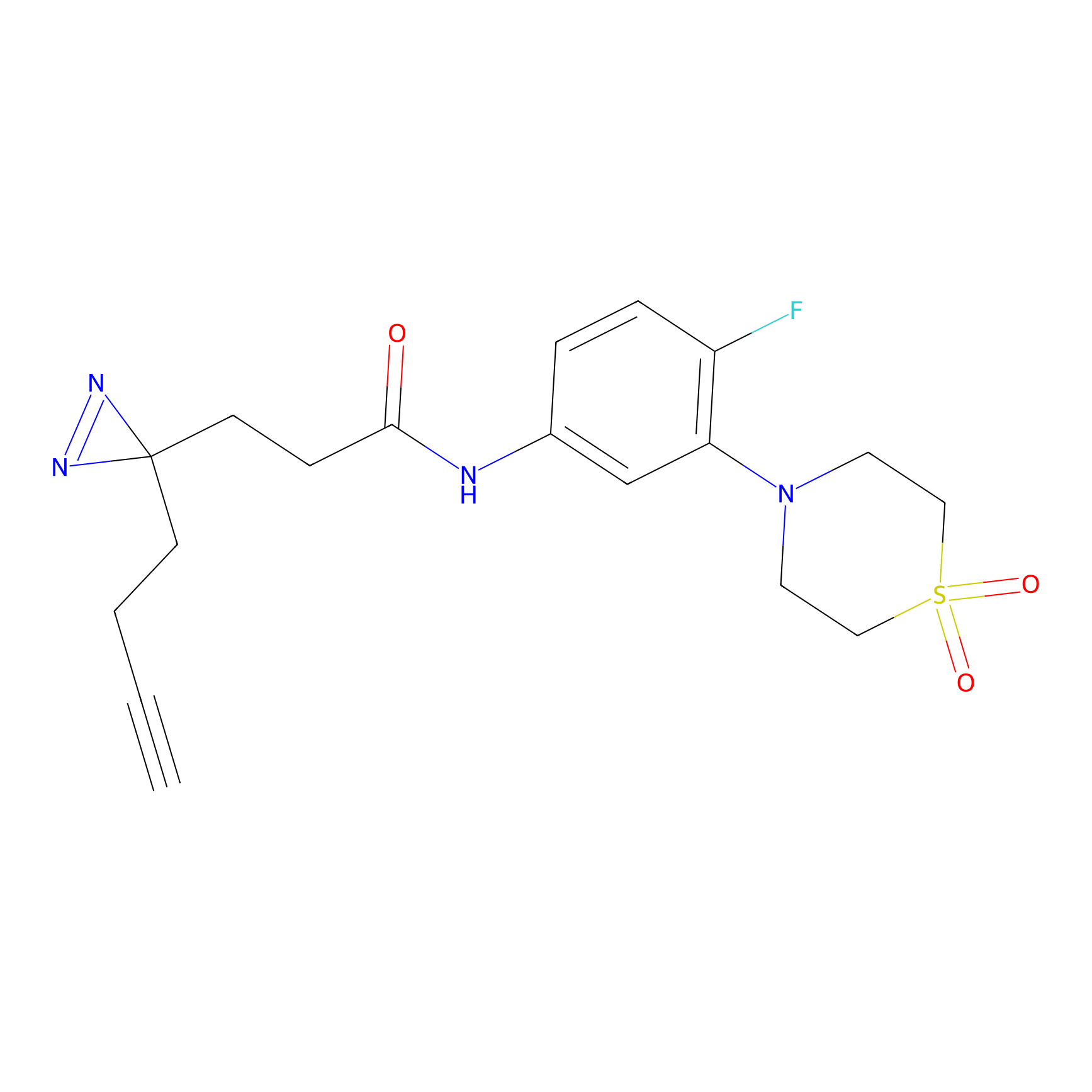
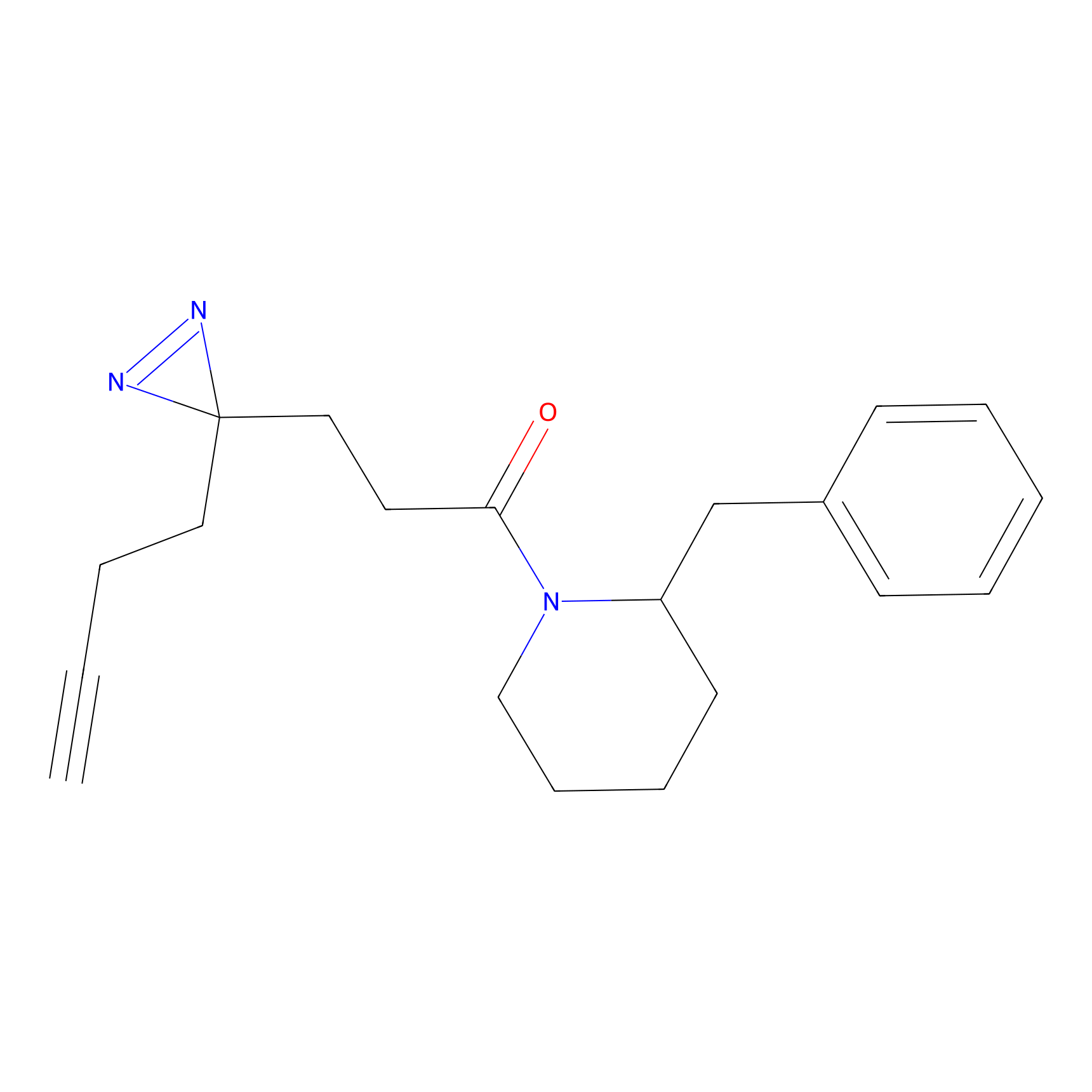
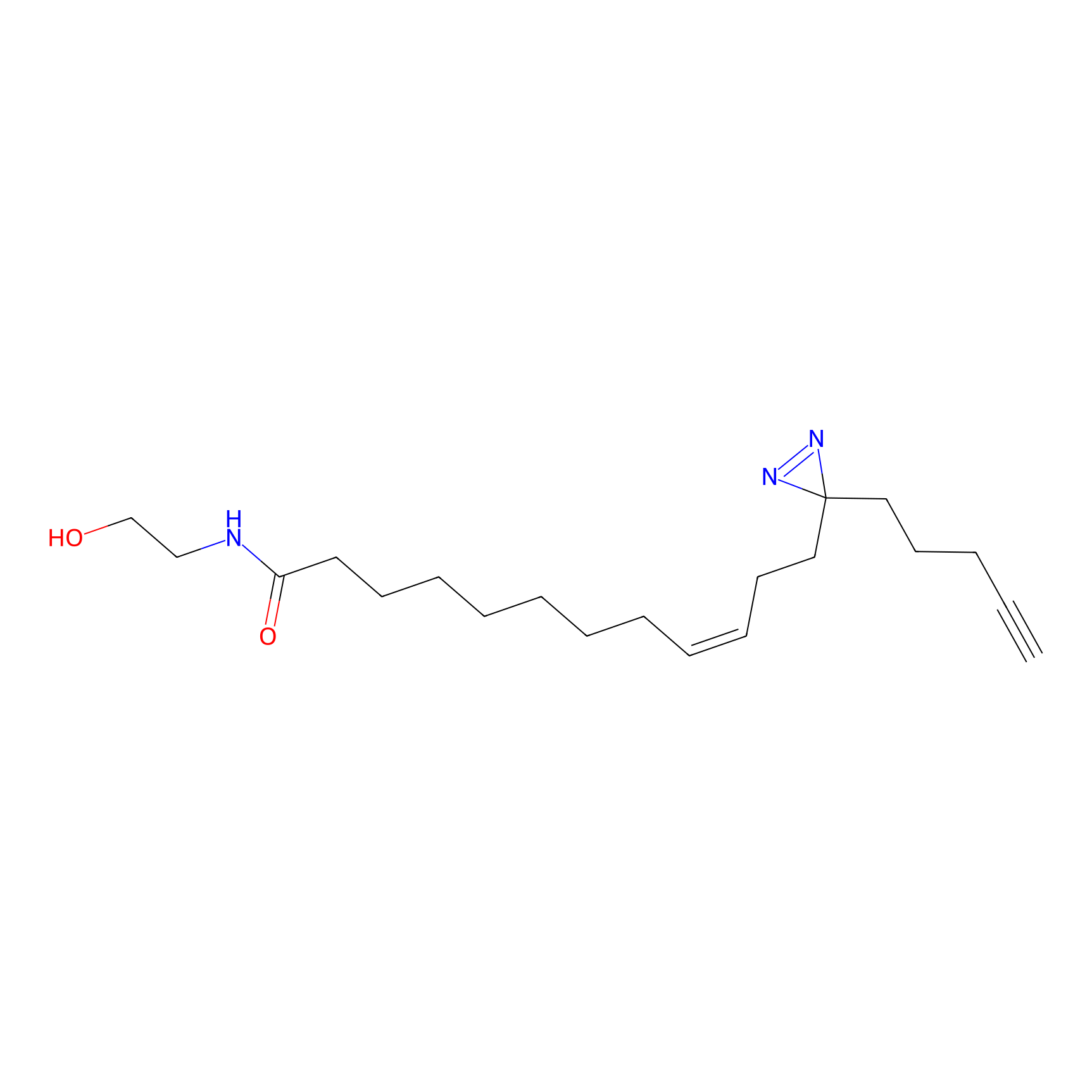
|
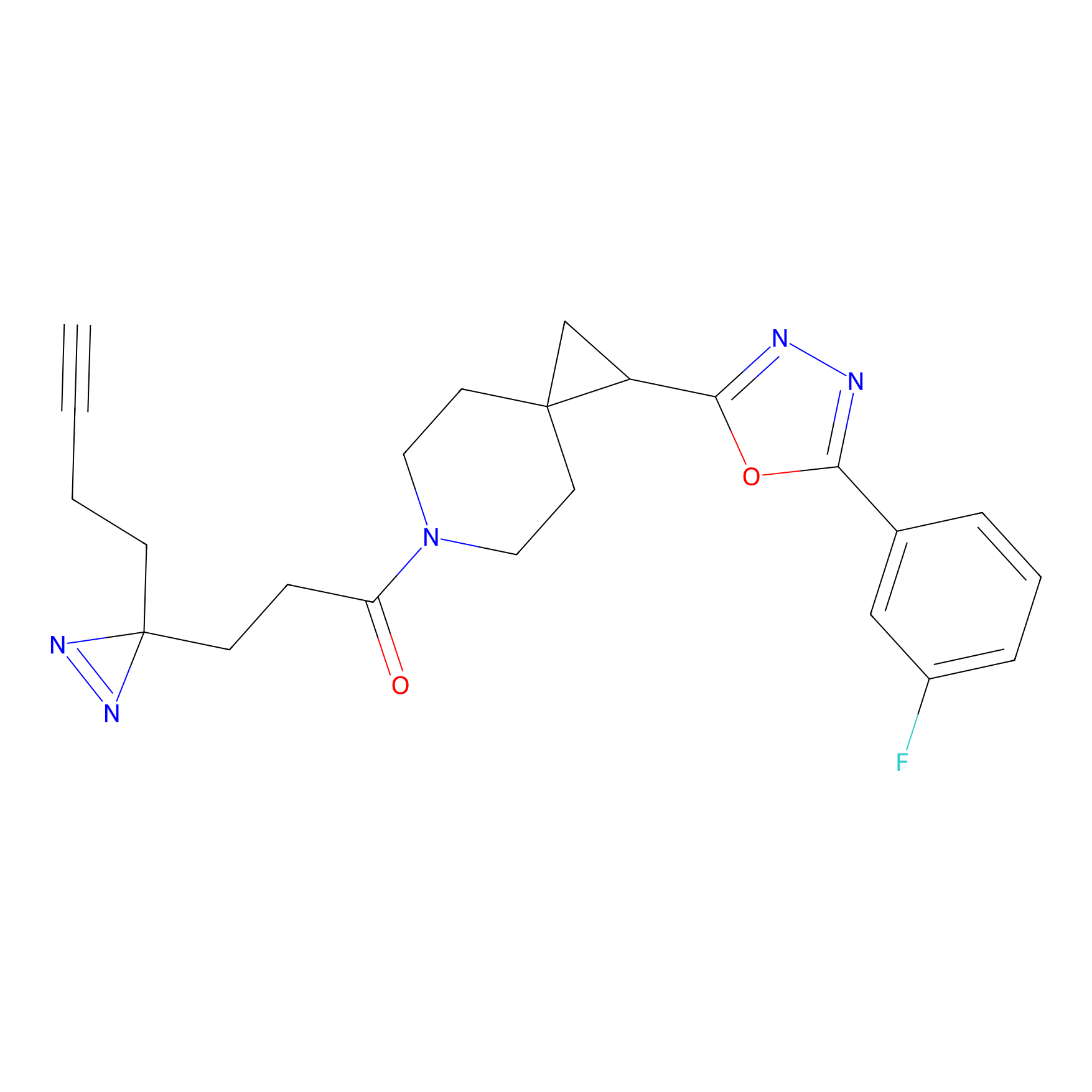
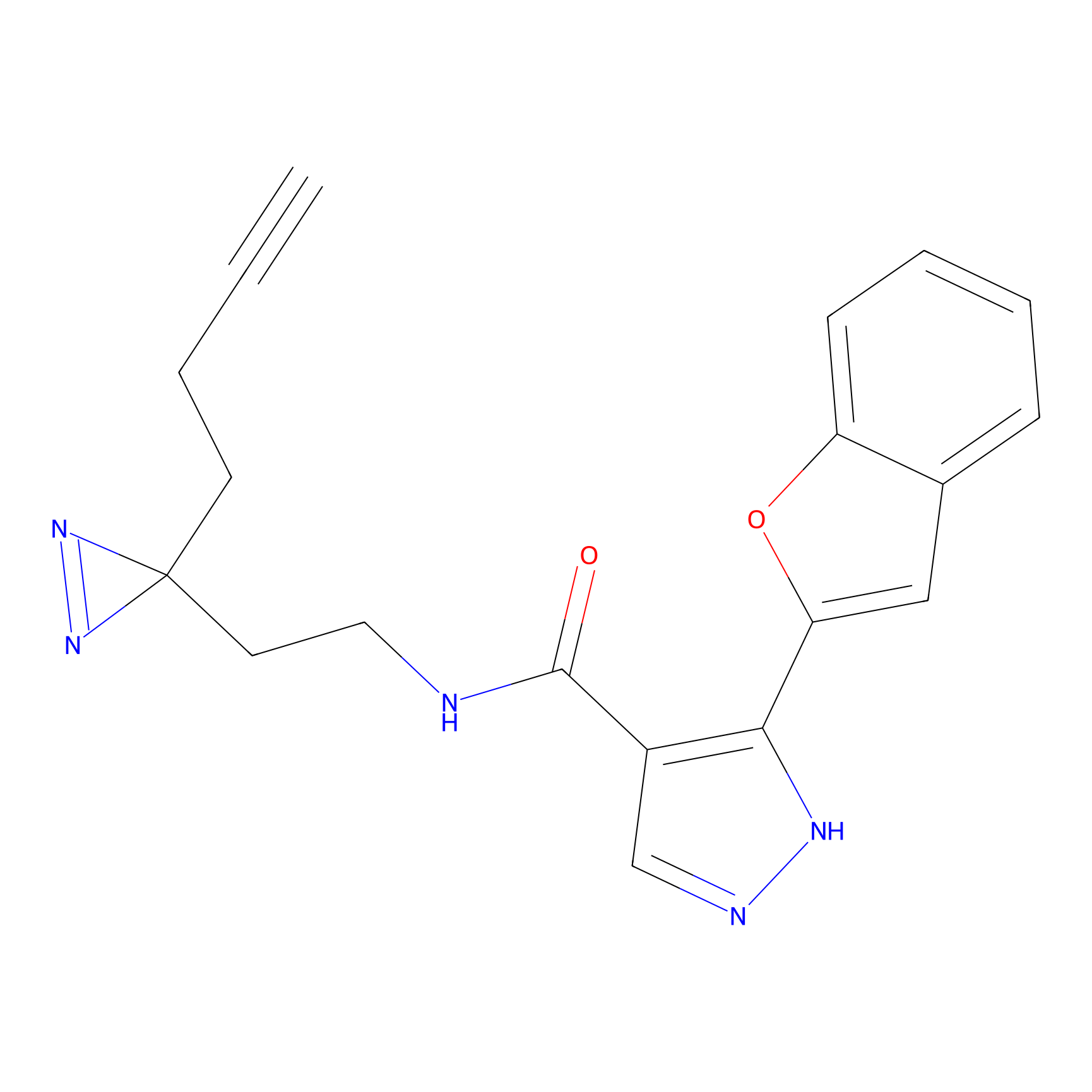
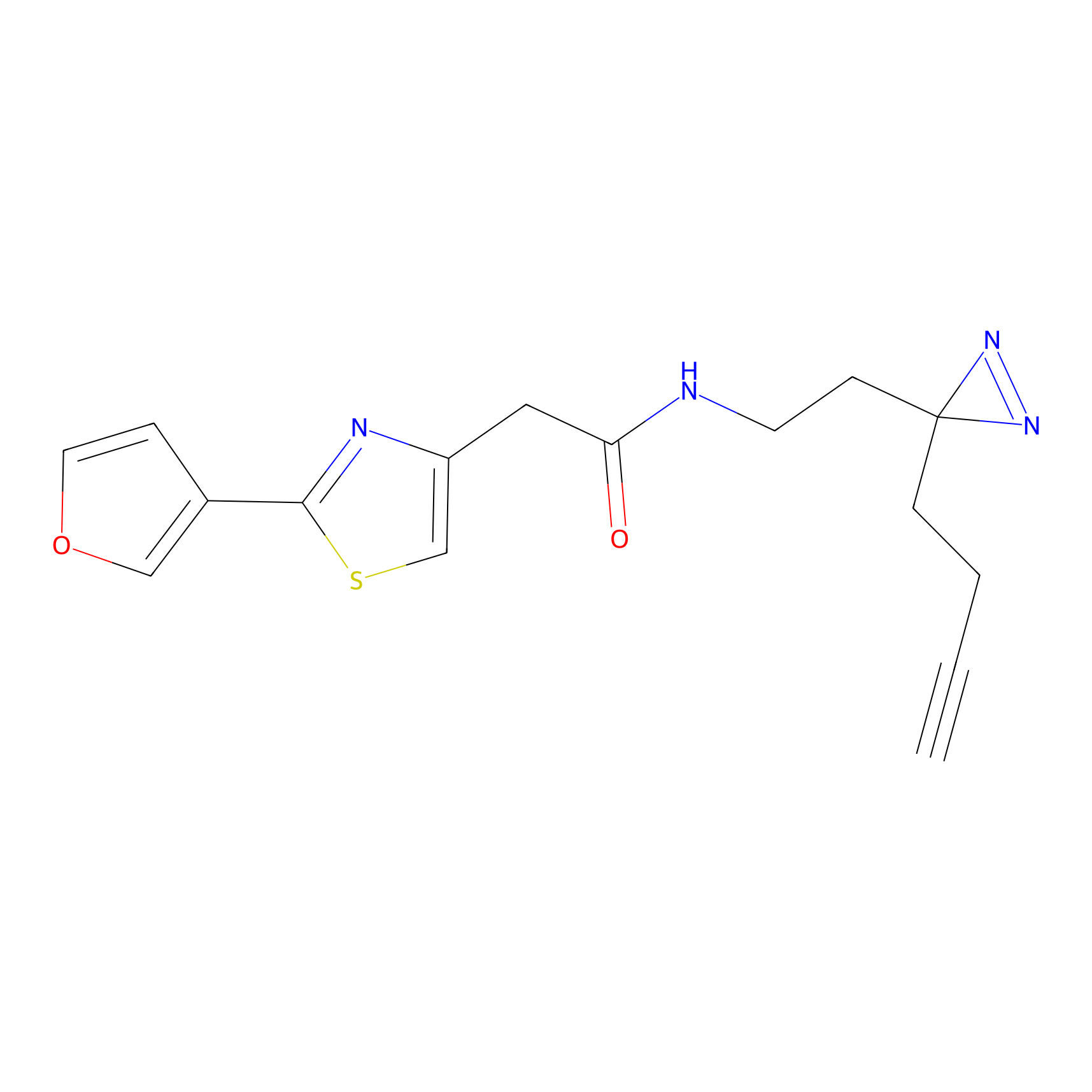
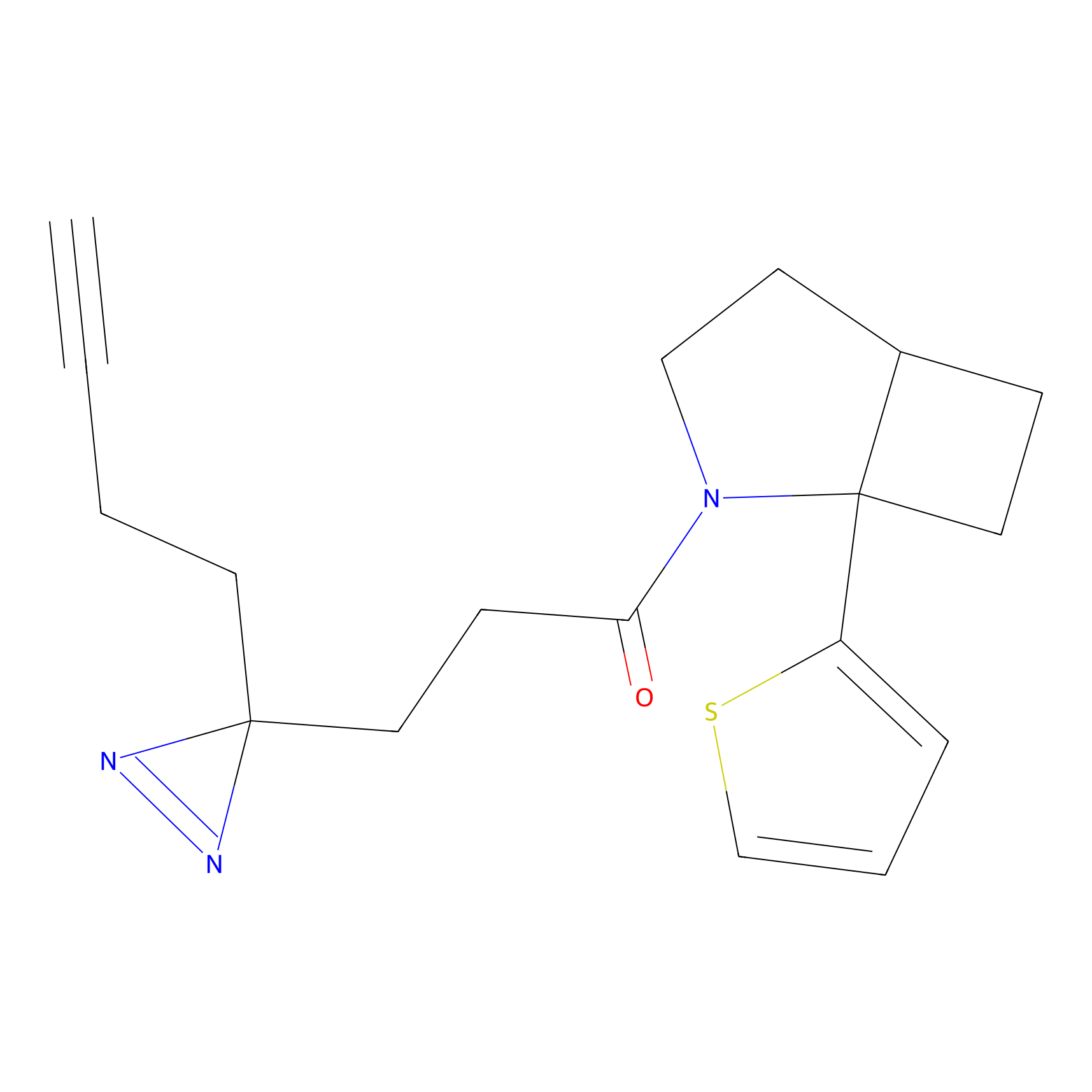
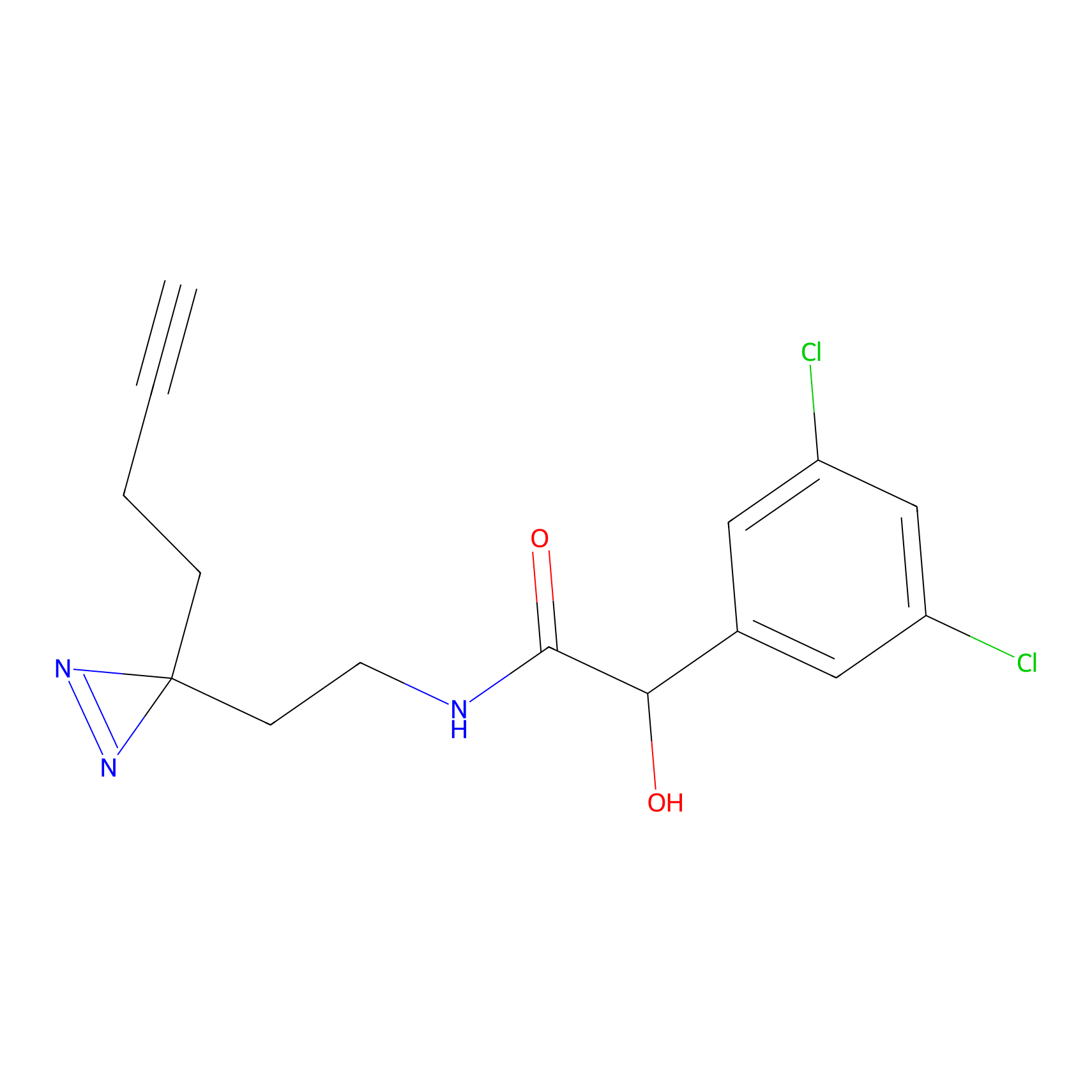
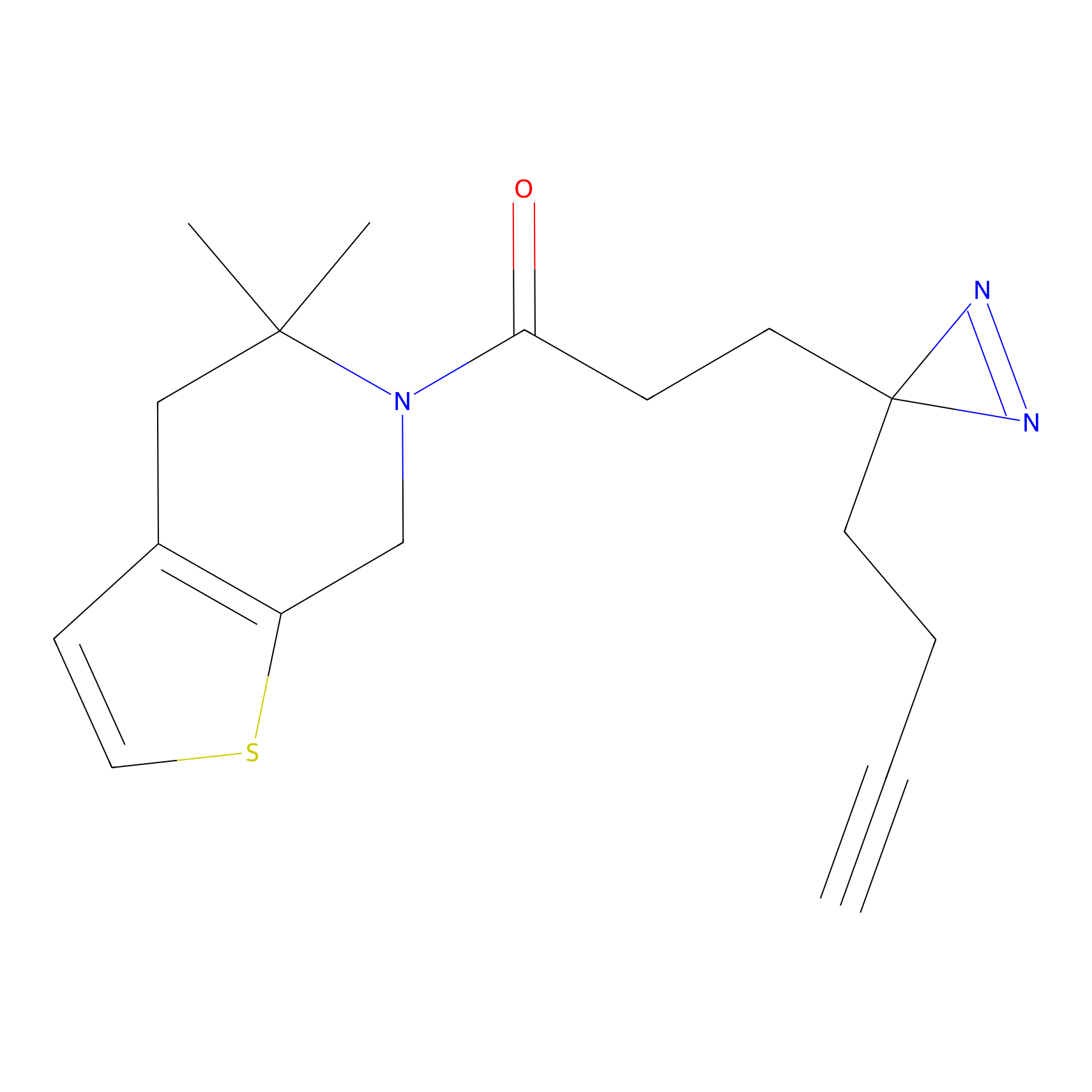
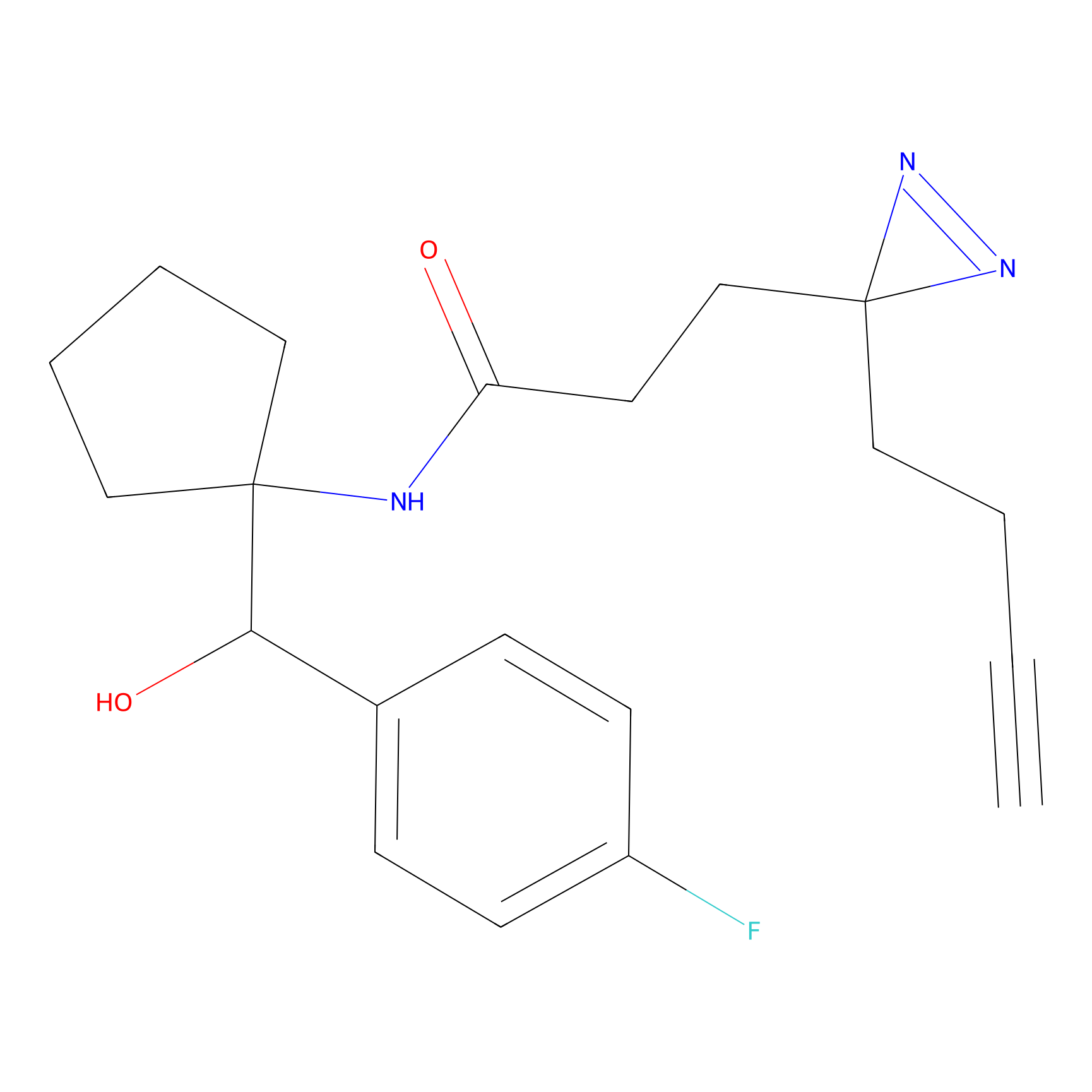
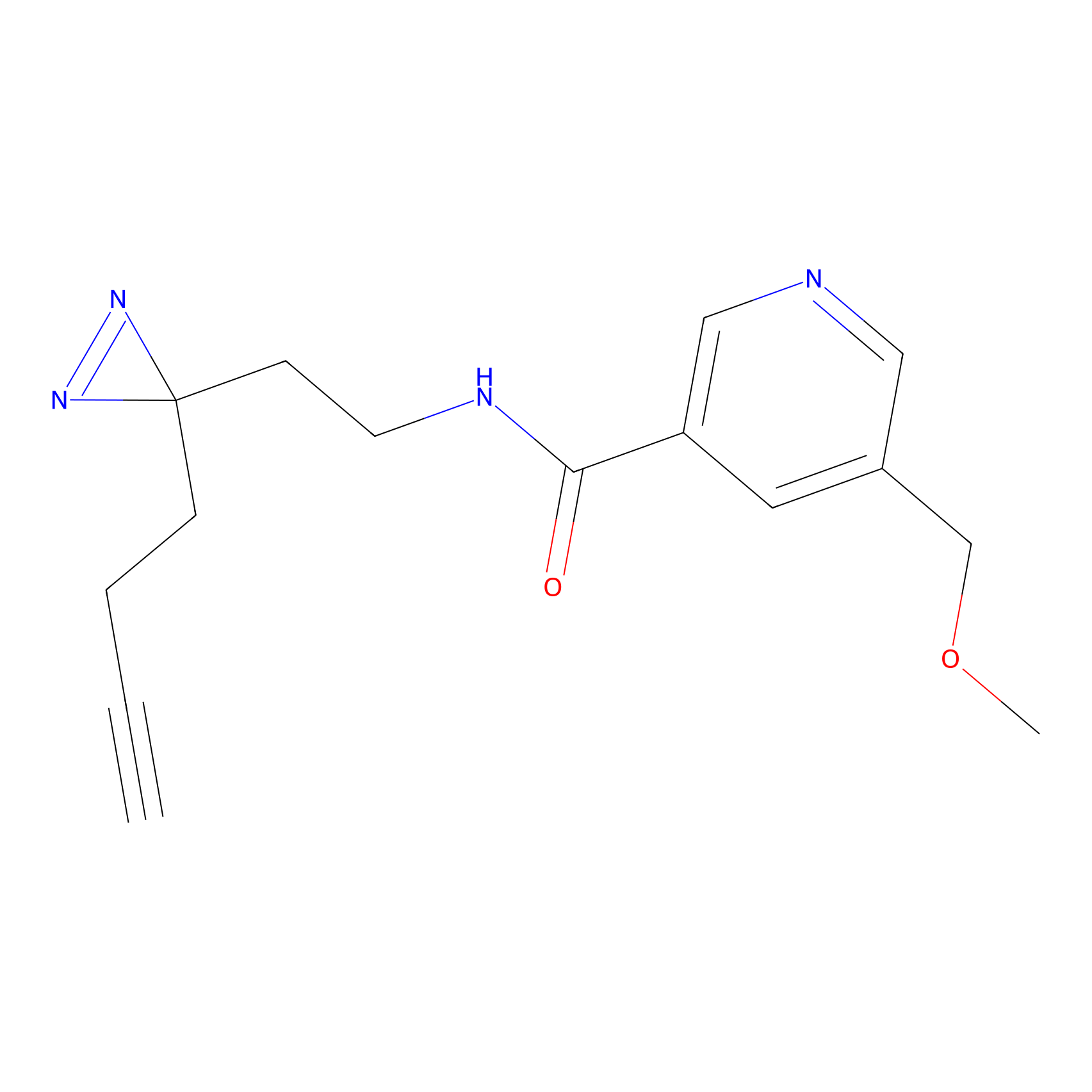
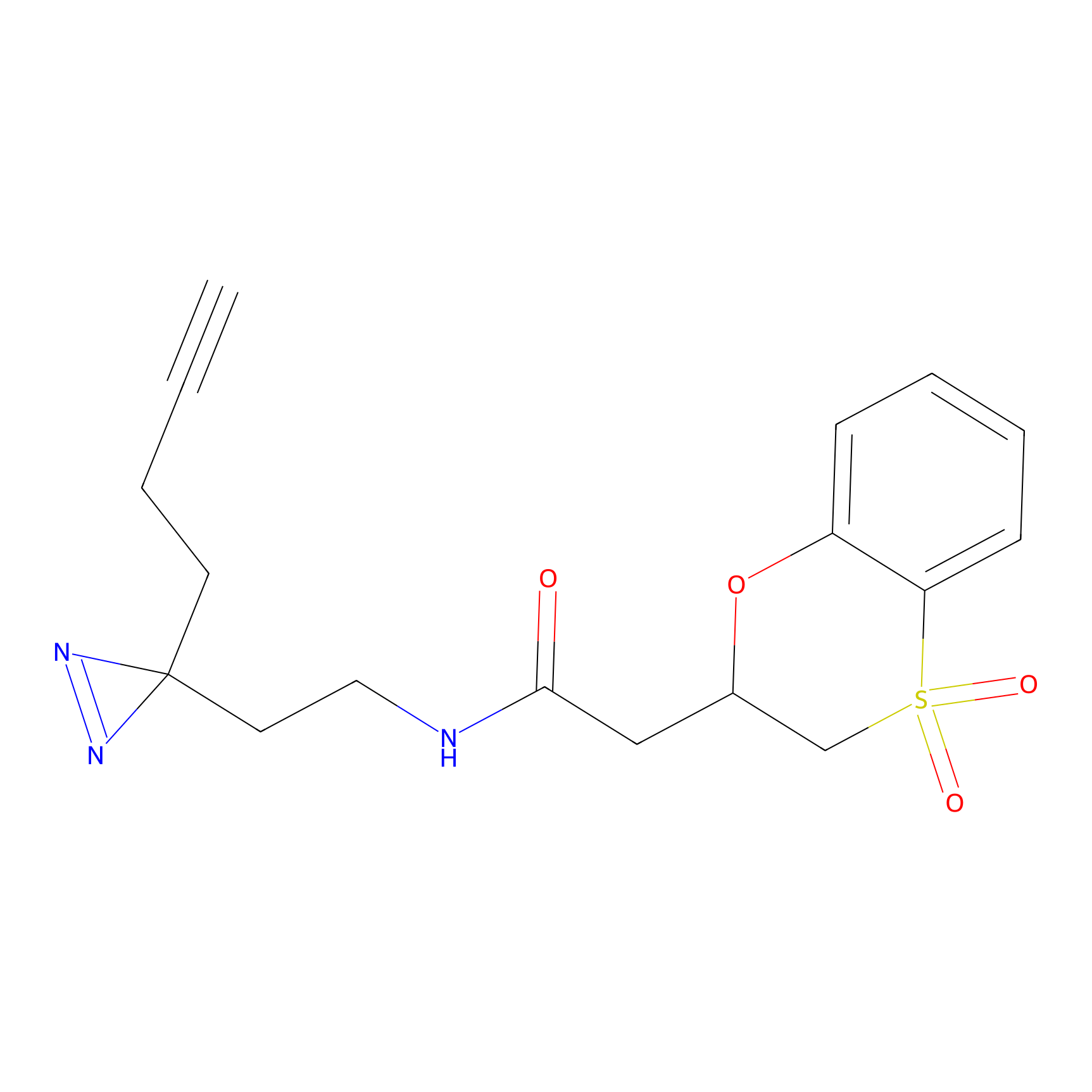
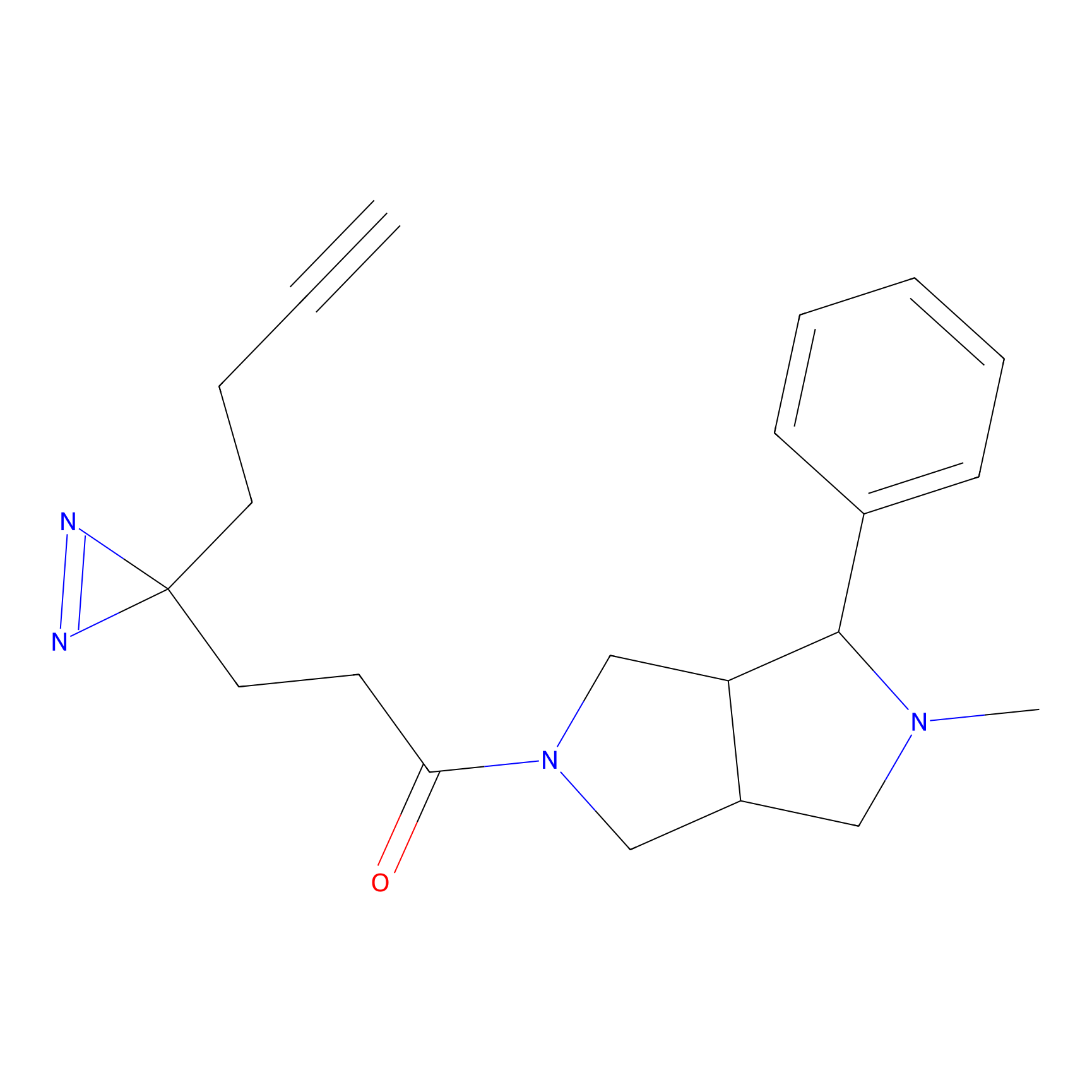
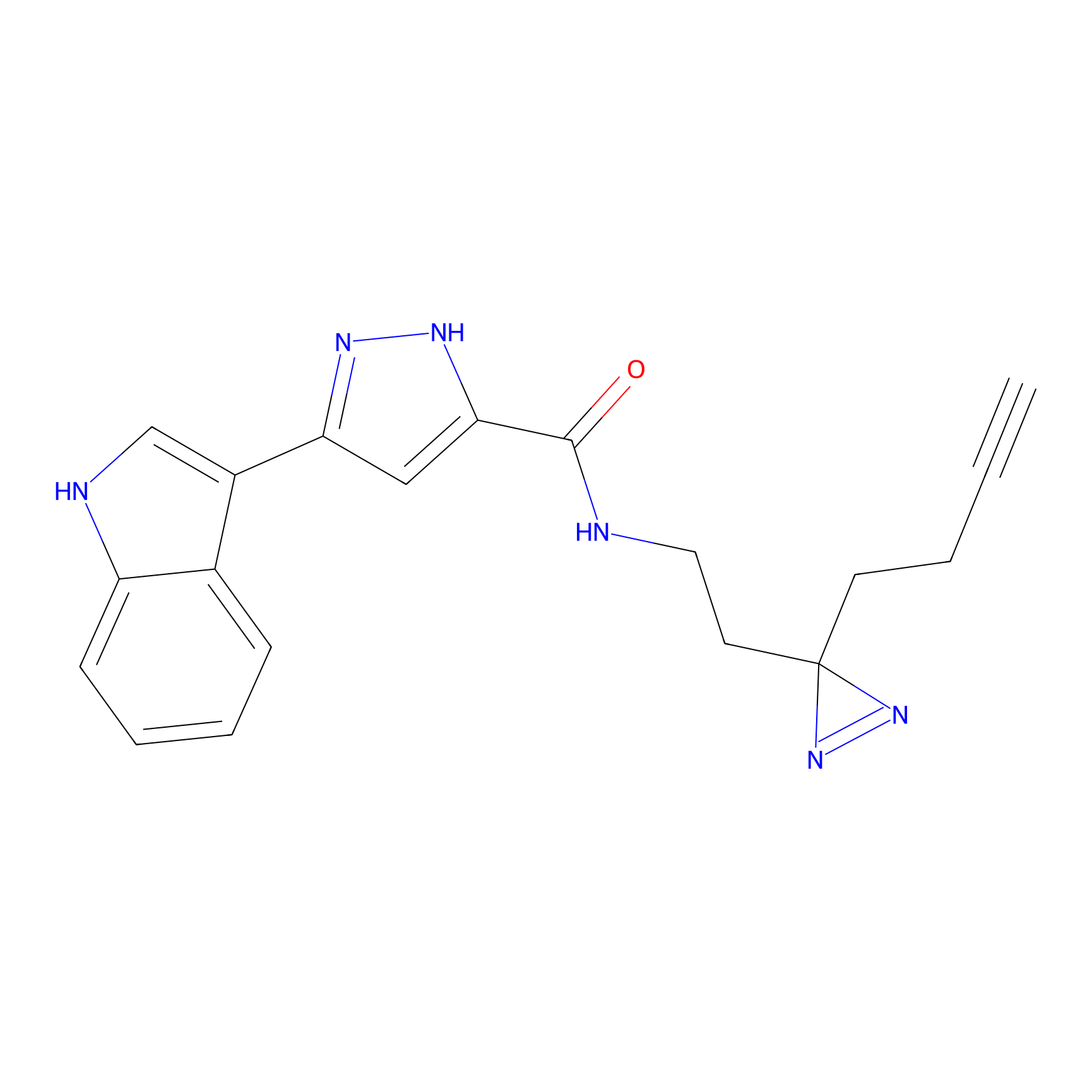
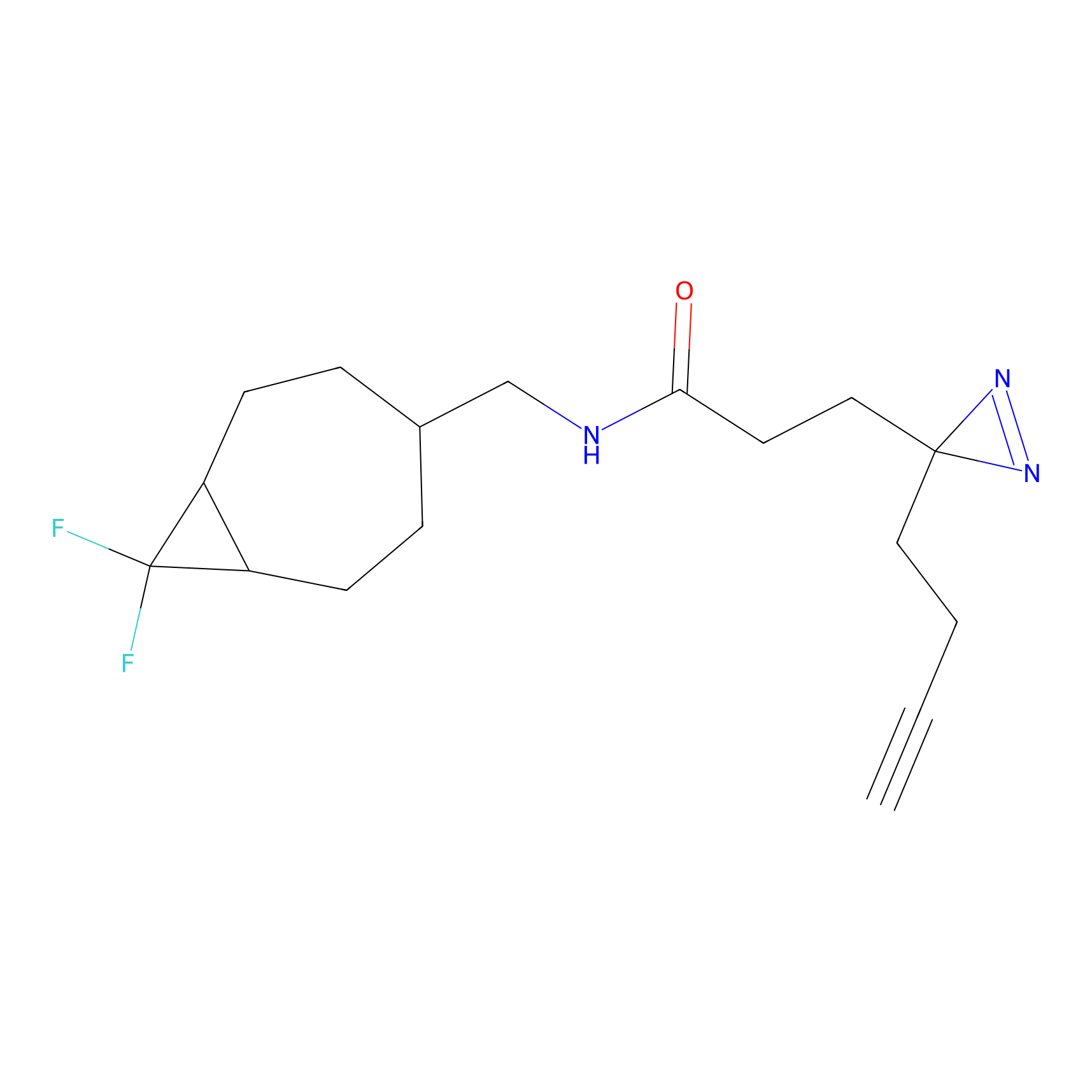
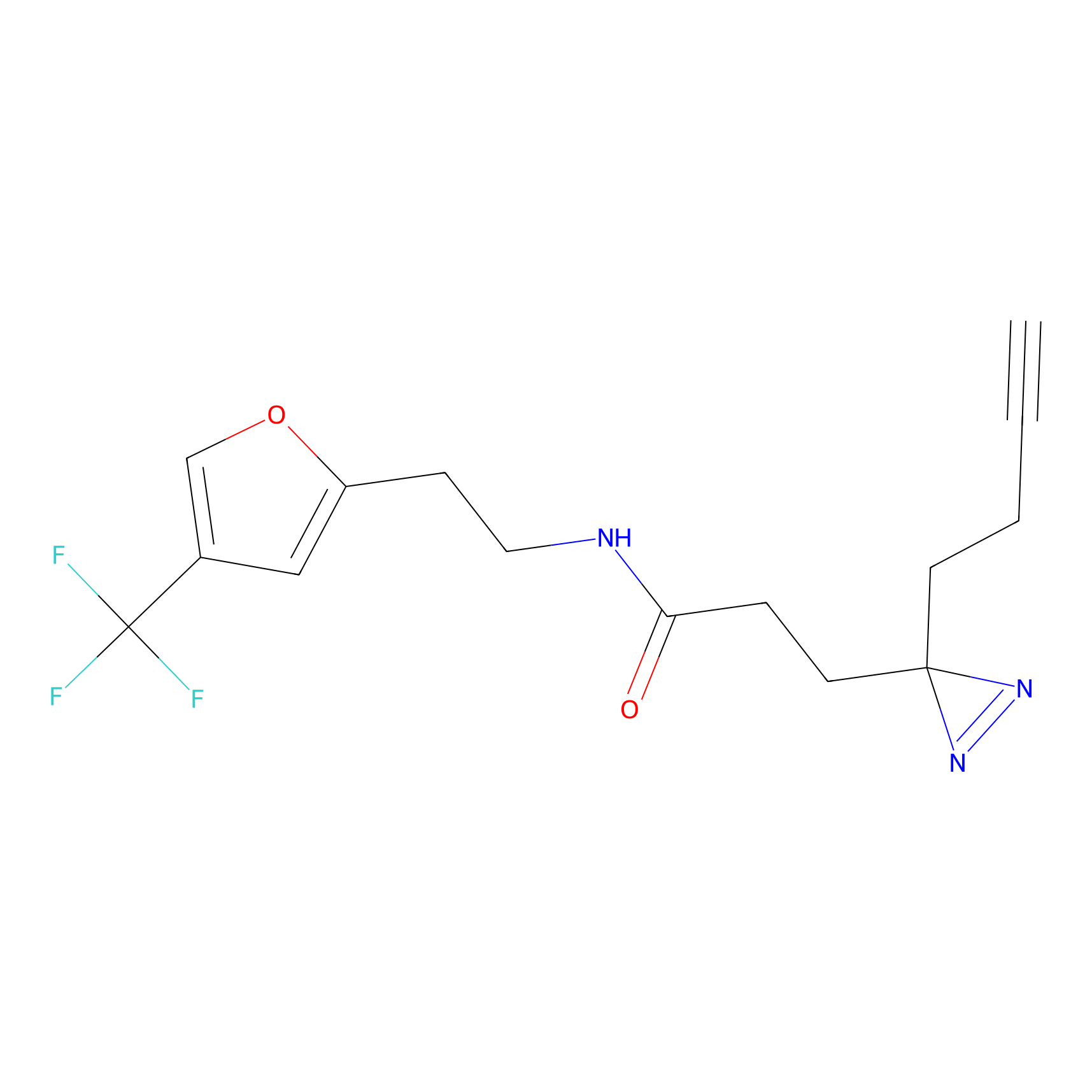
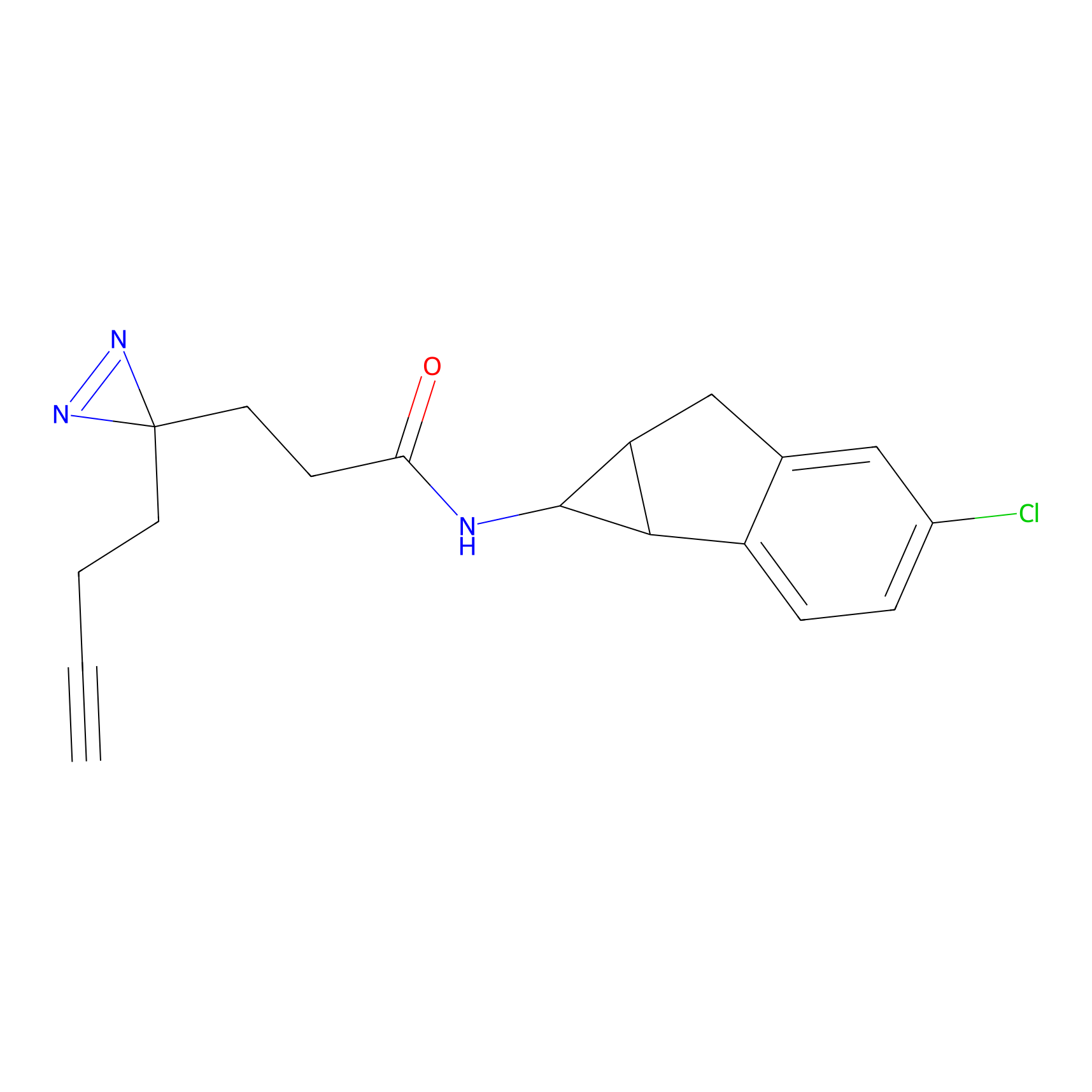
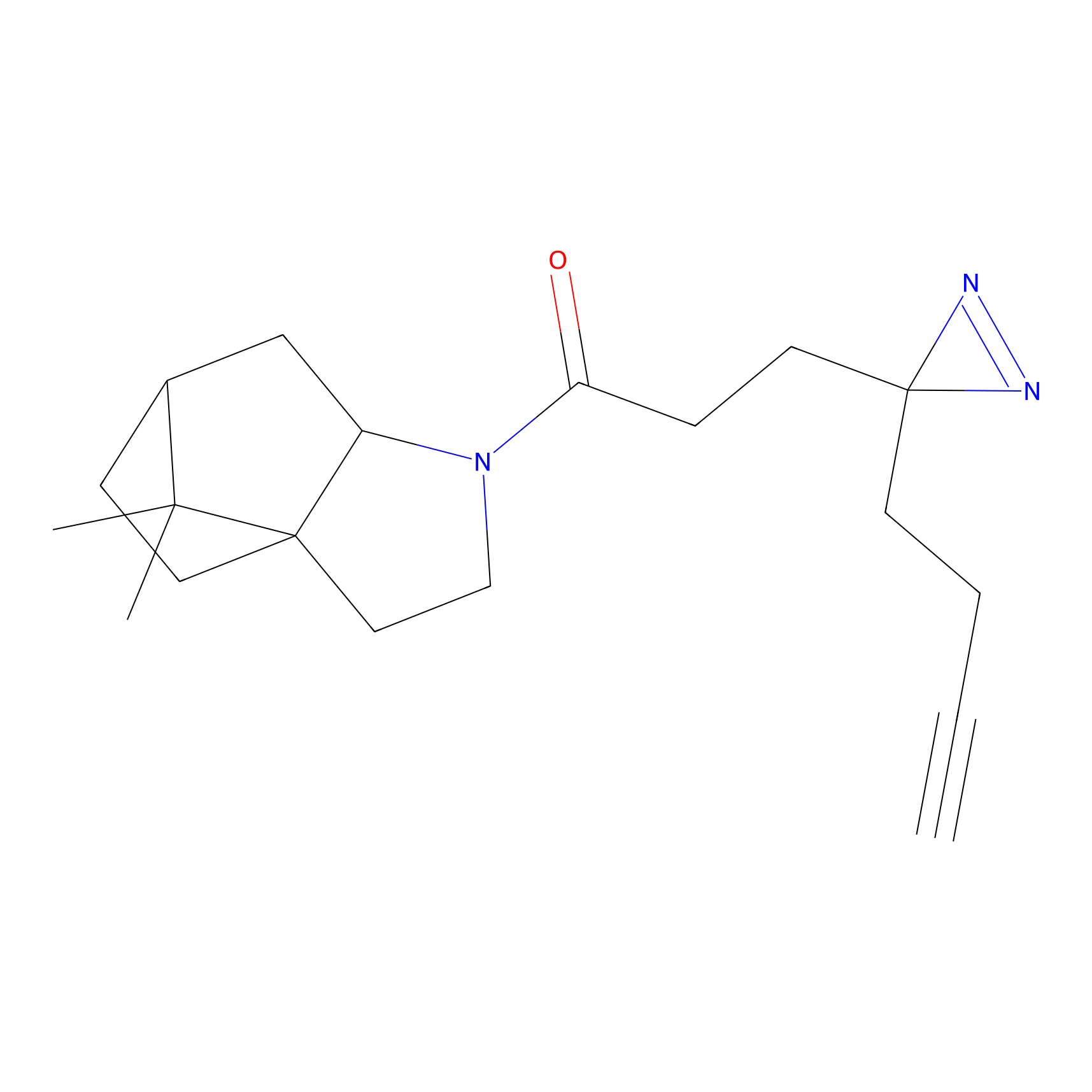
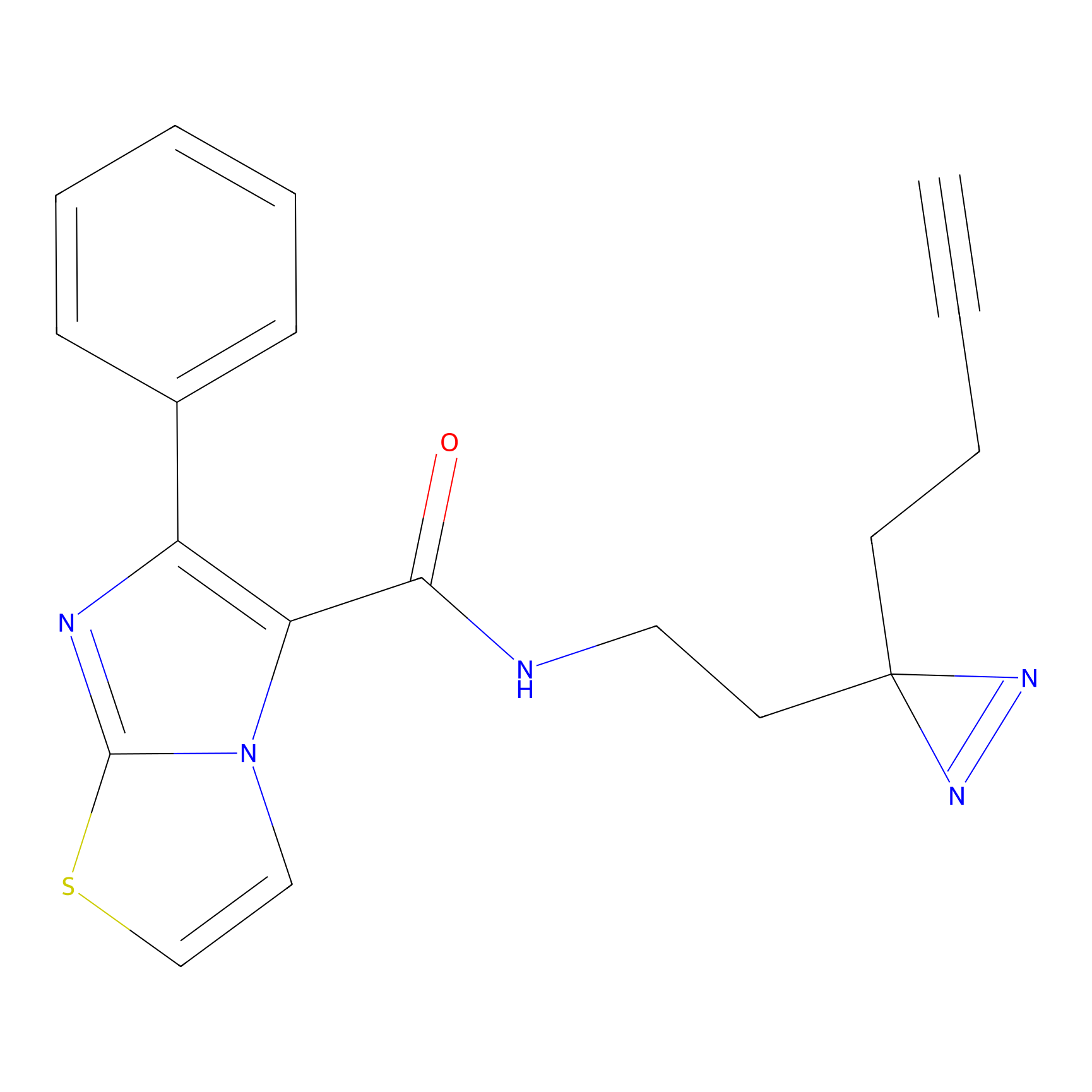
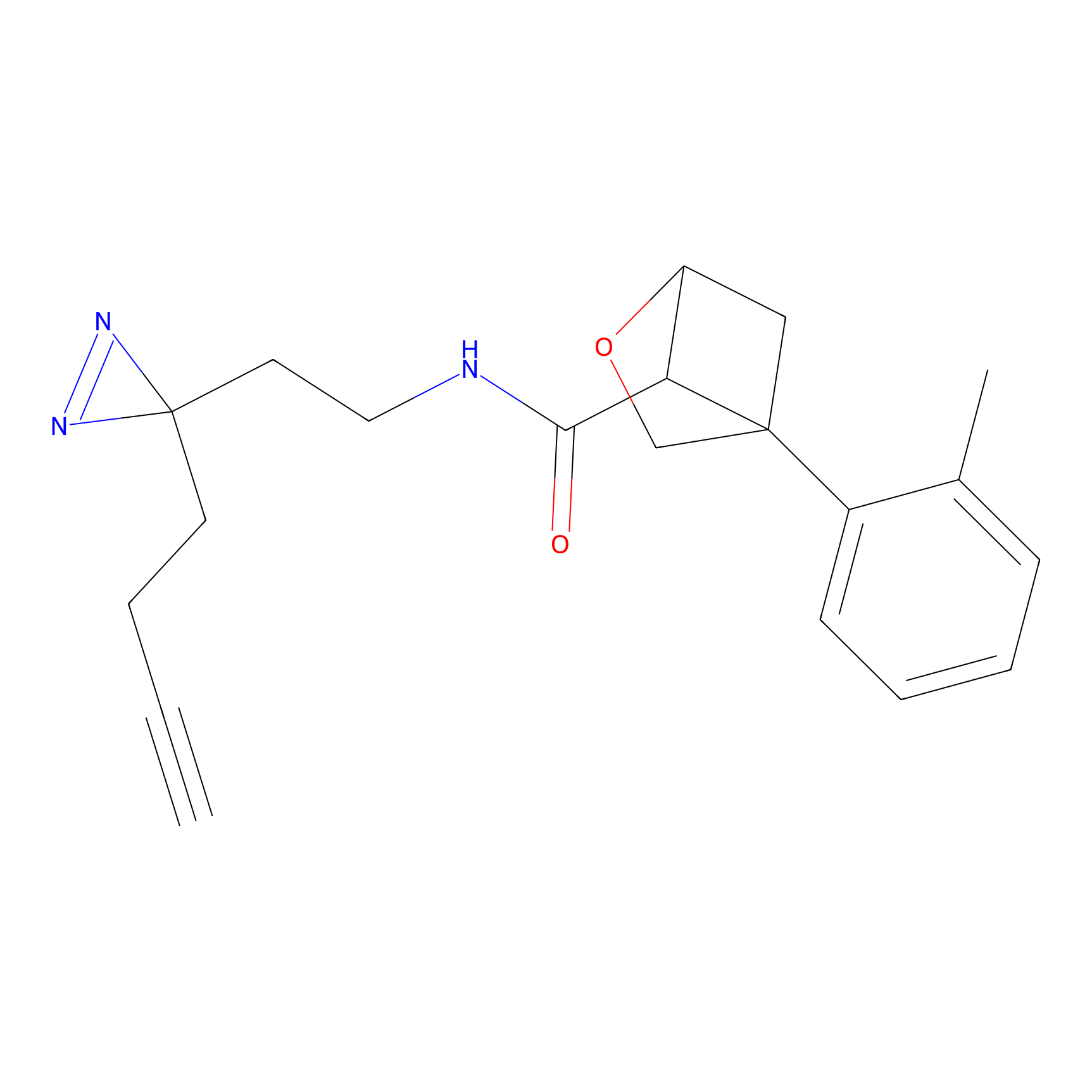
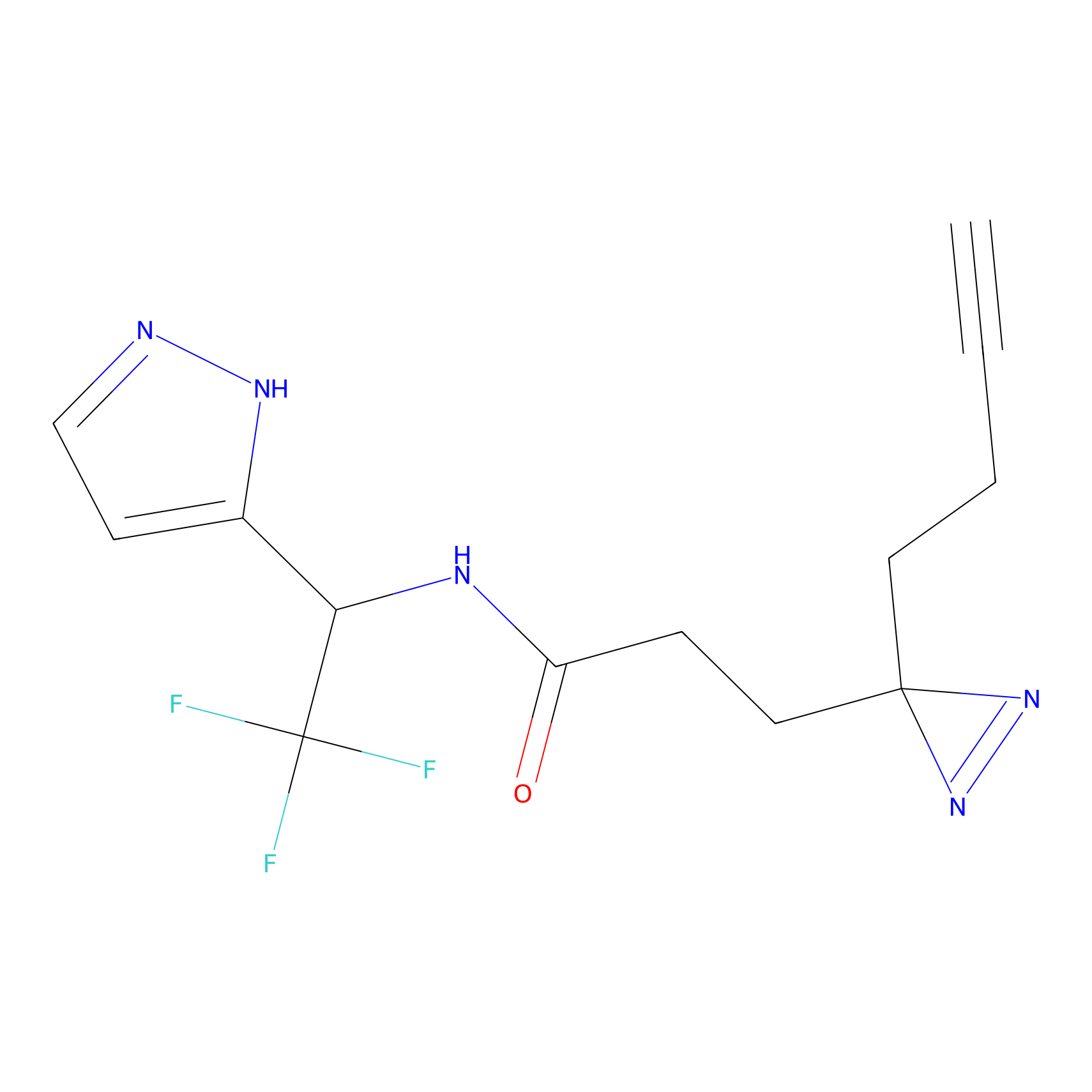
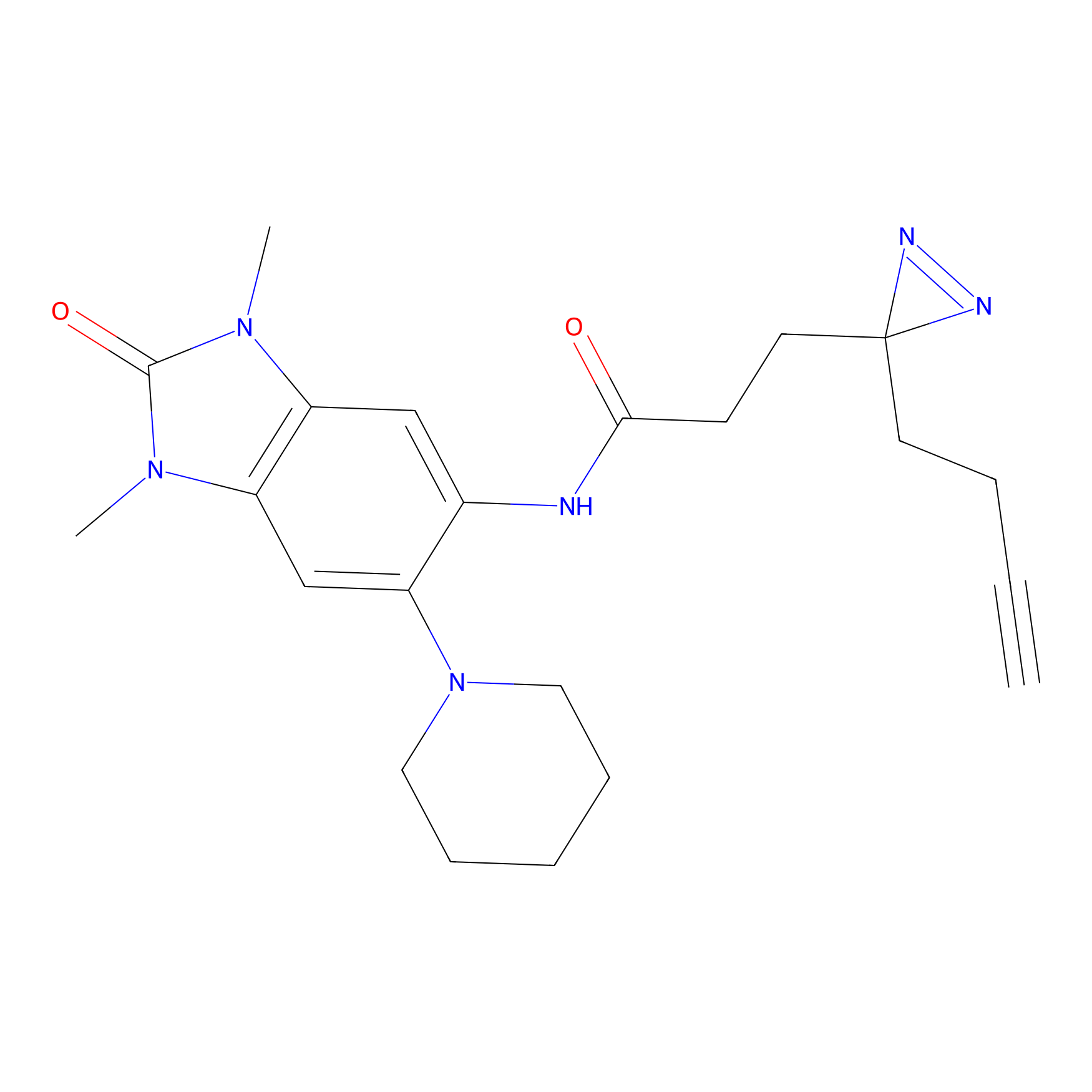
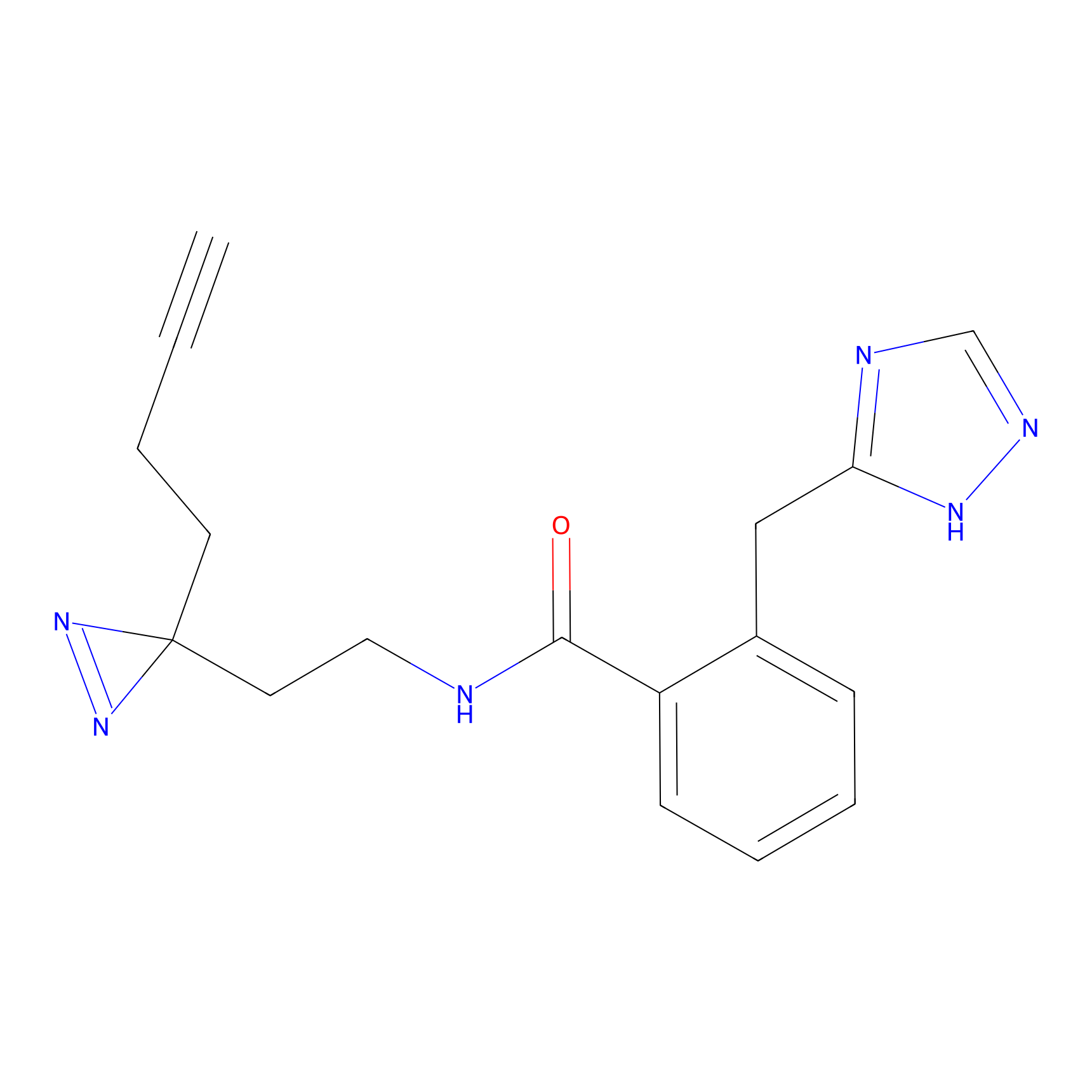
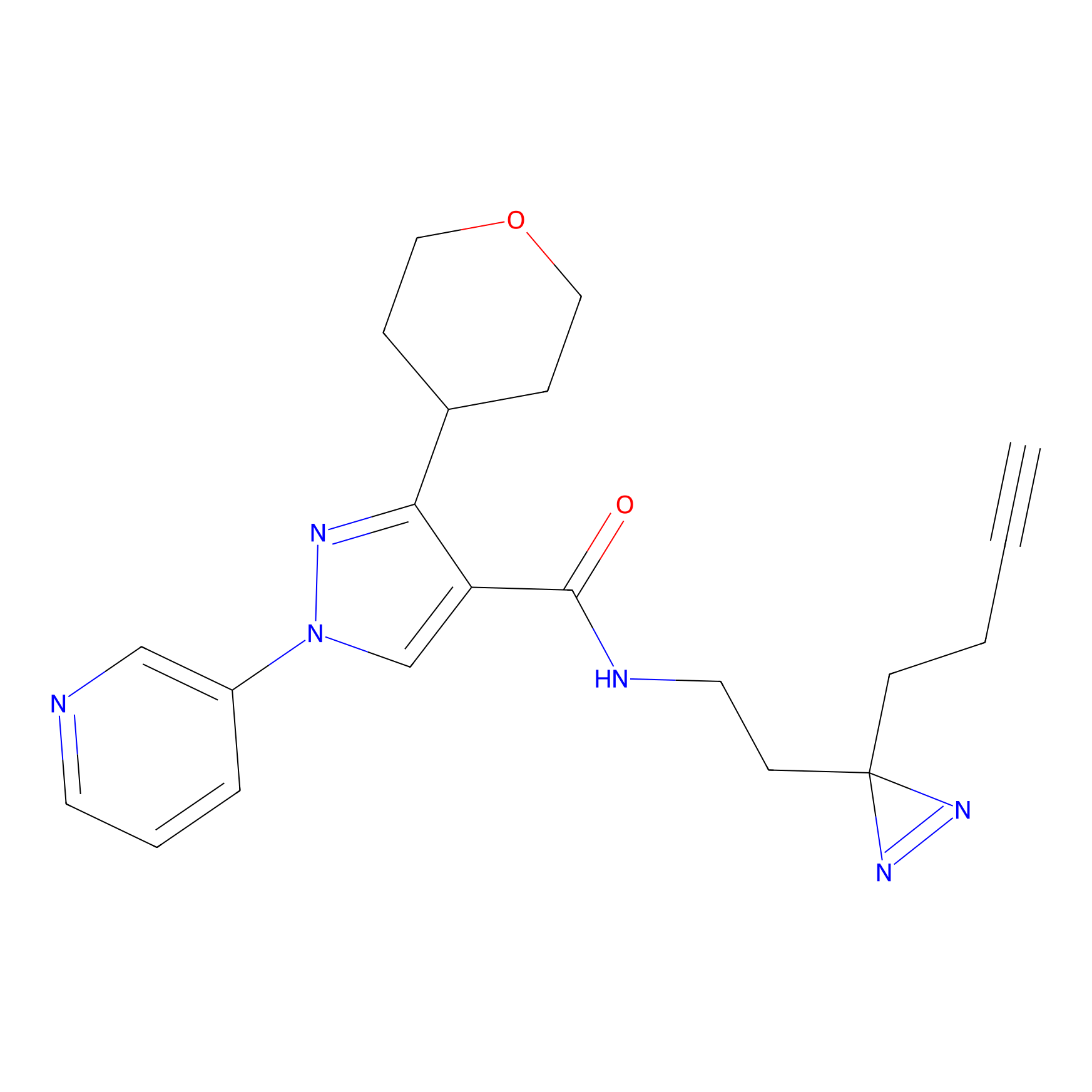
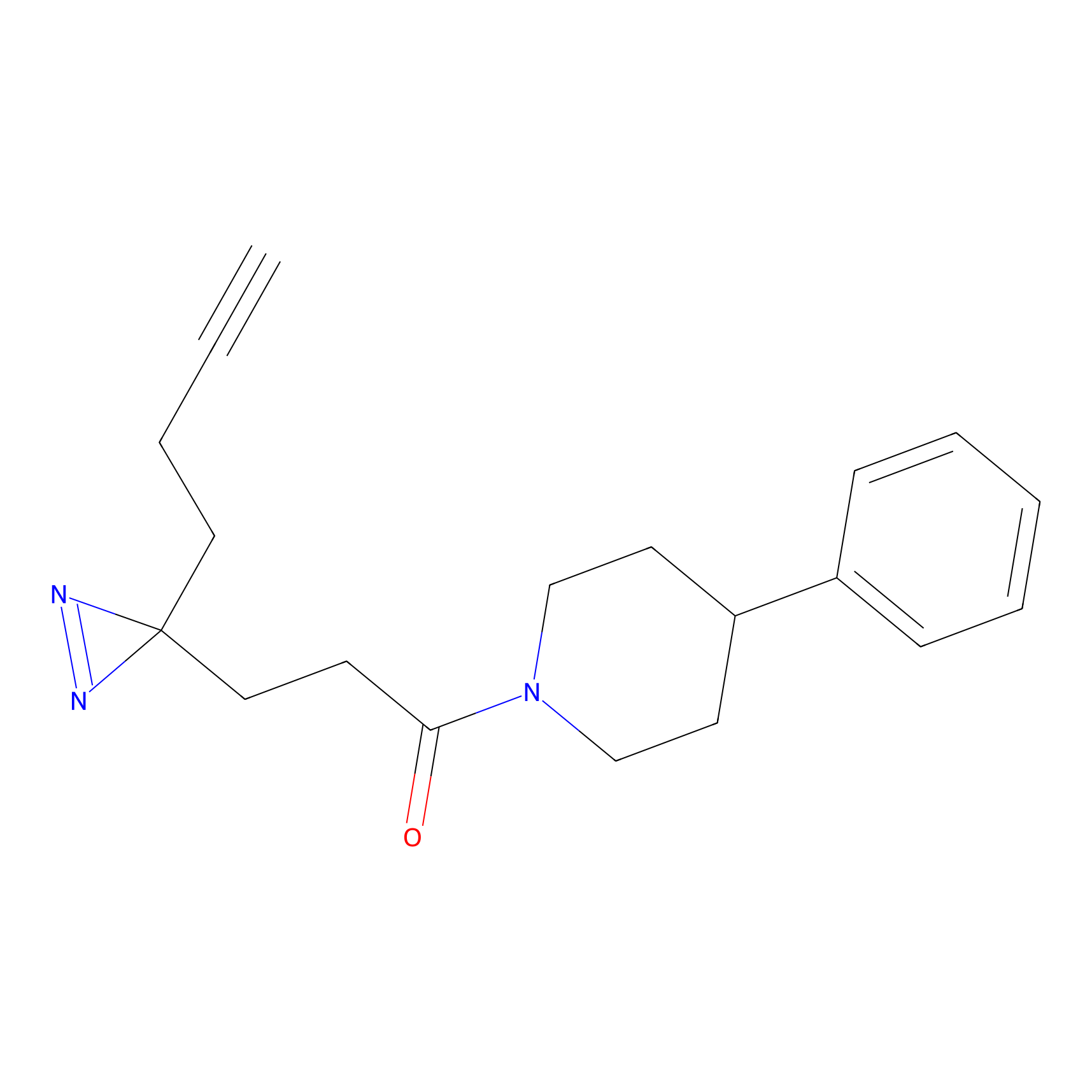
STPyne Probe Info |
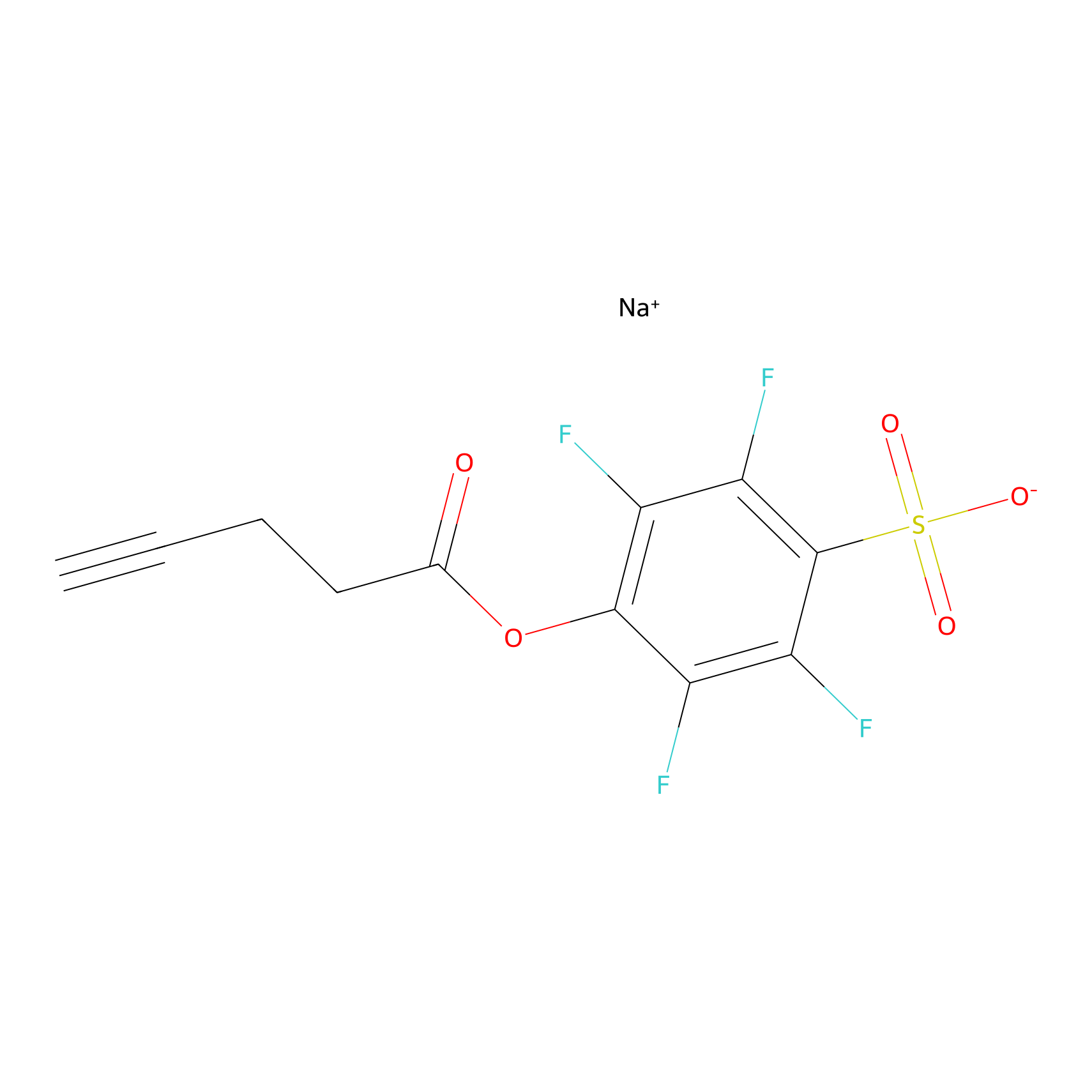 |
K144(4.91) | LDD0277 | [3] | |
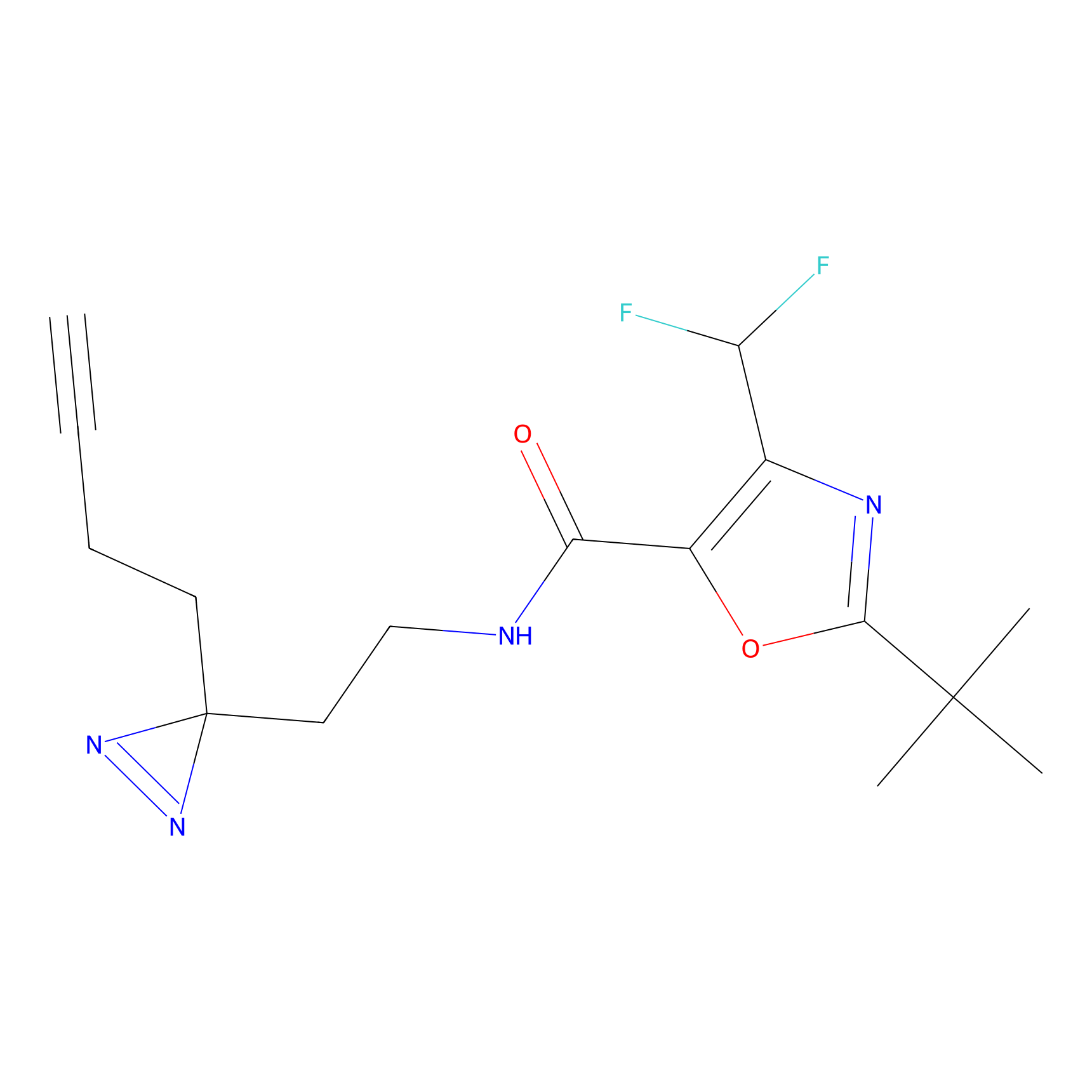
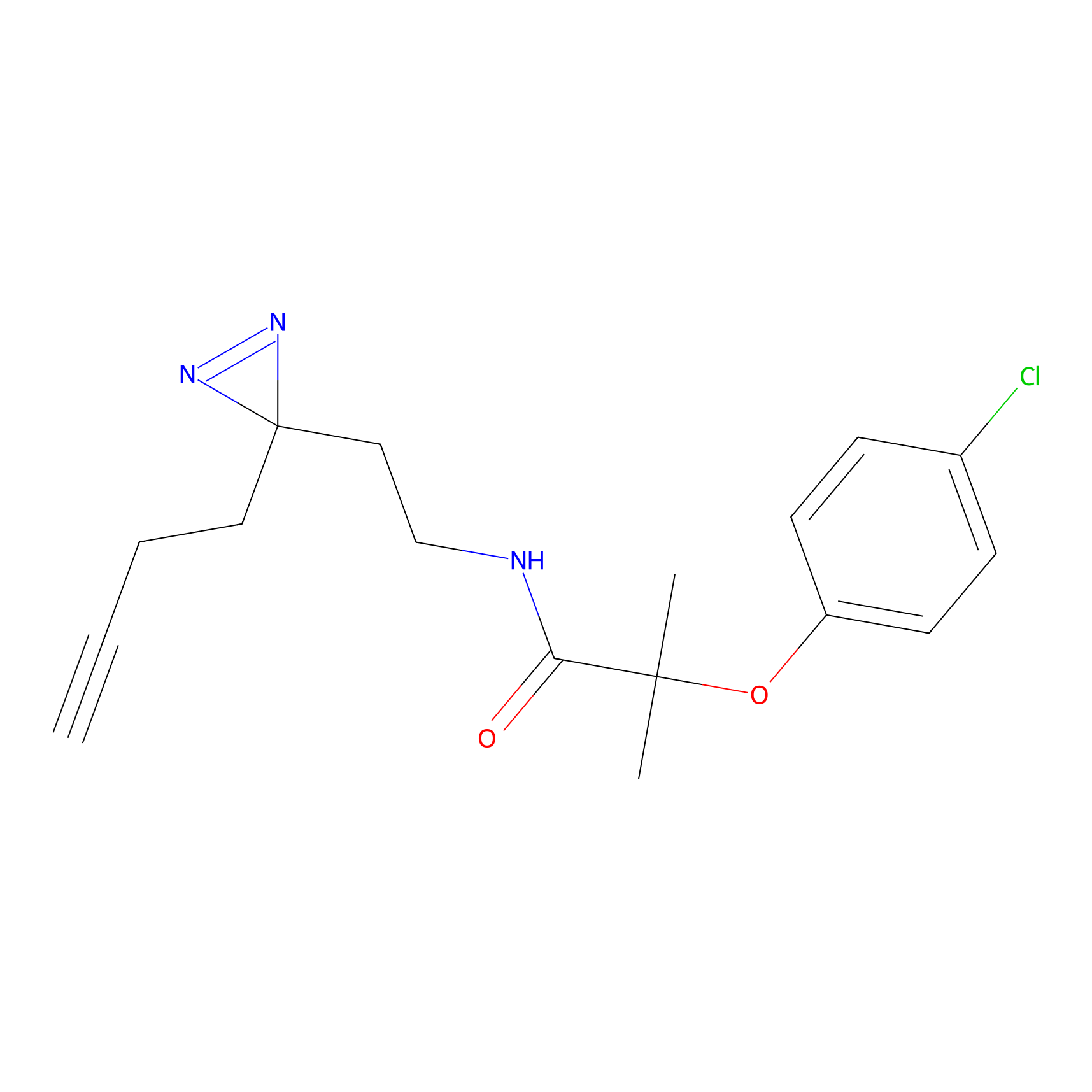
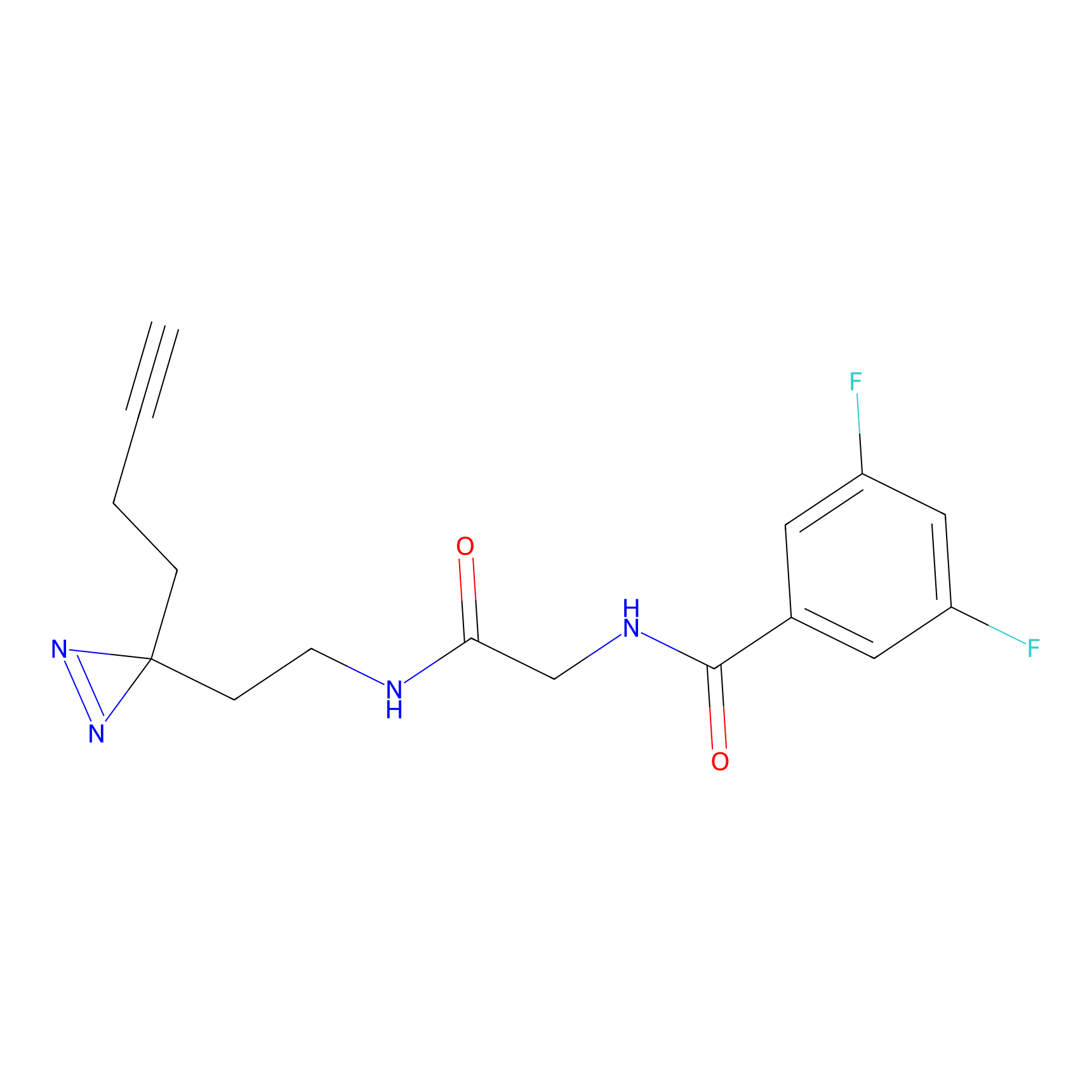
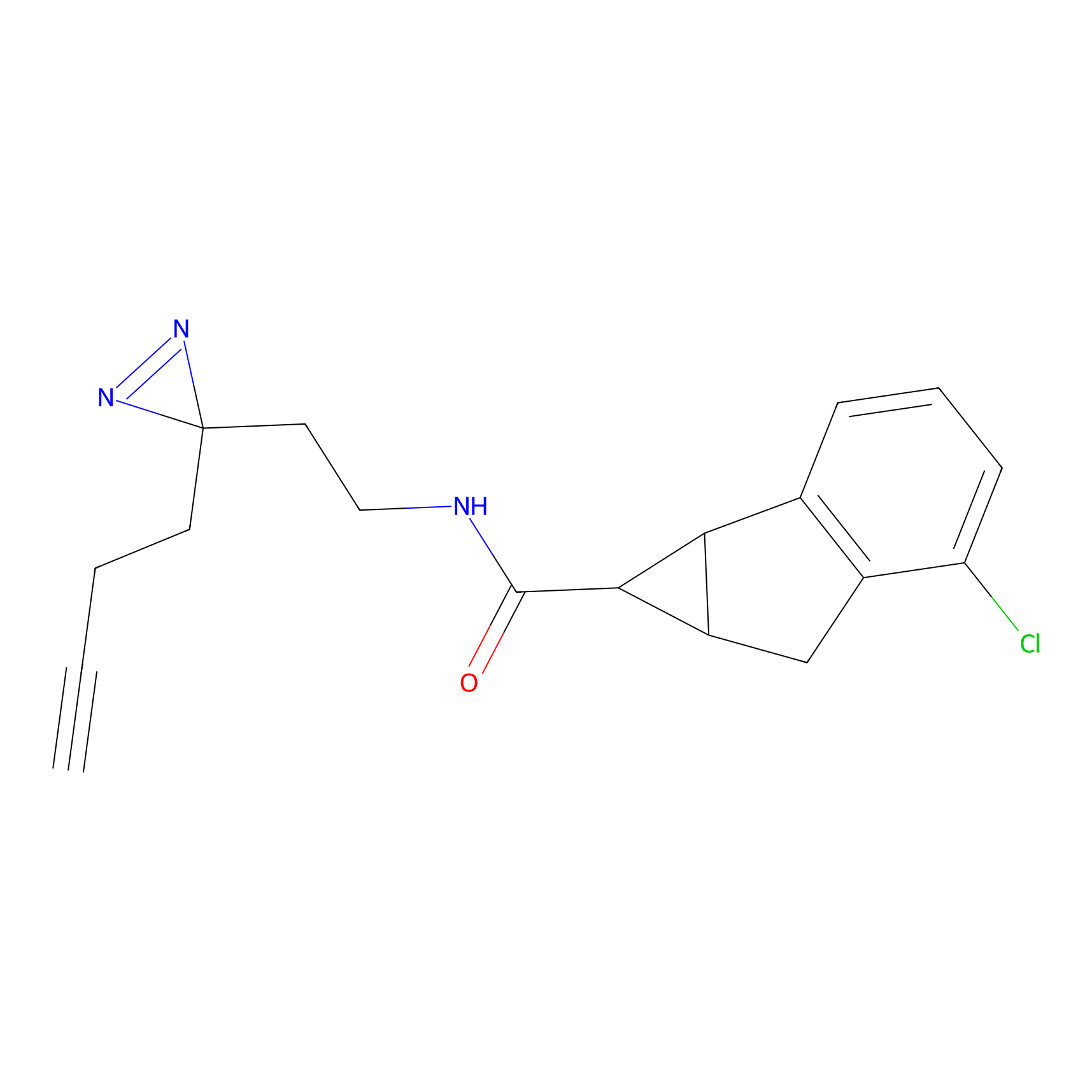
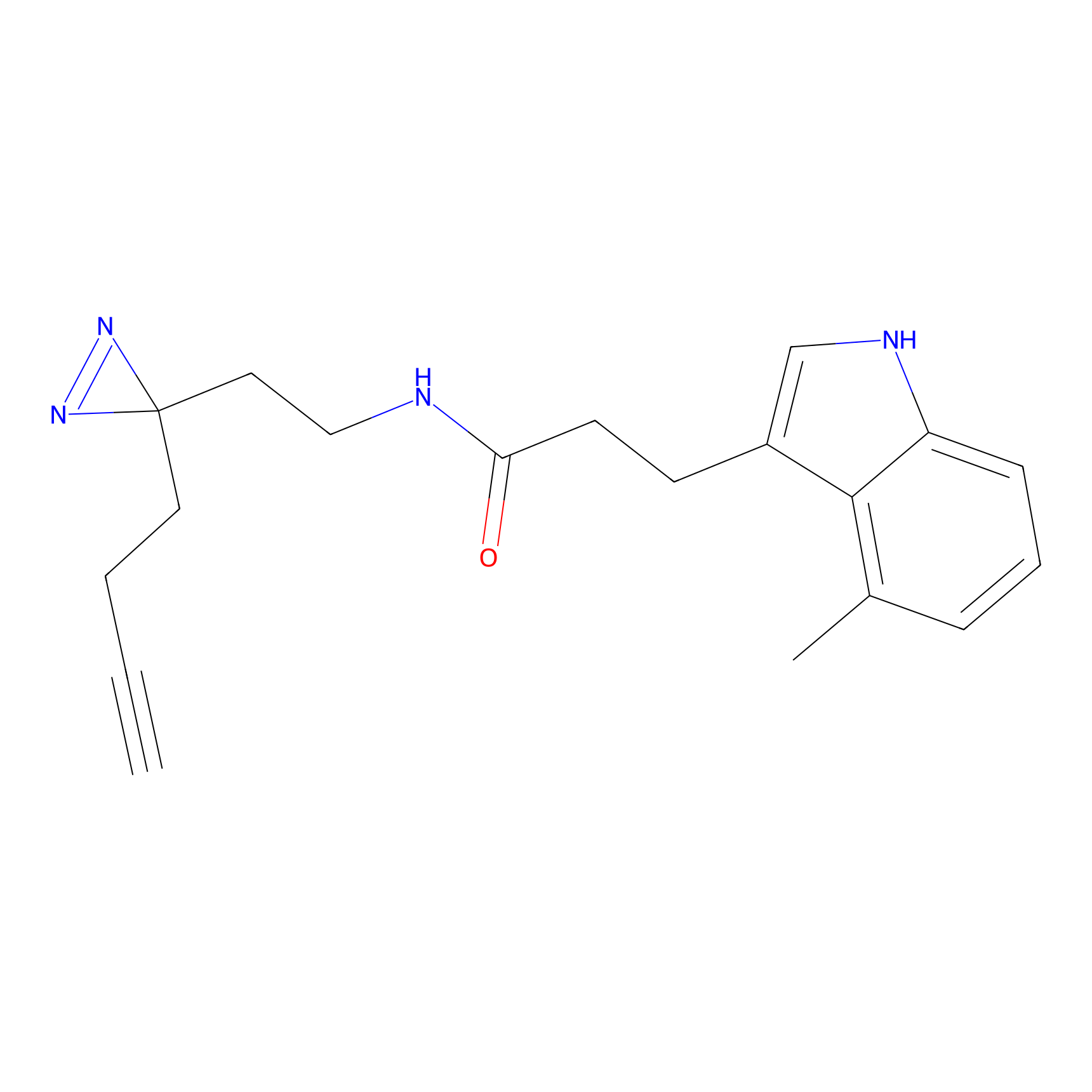
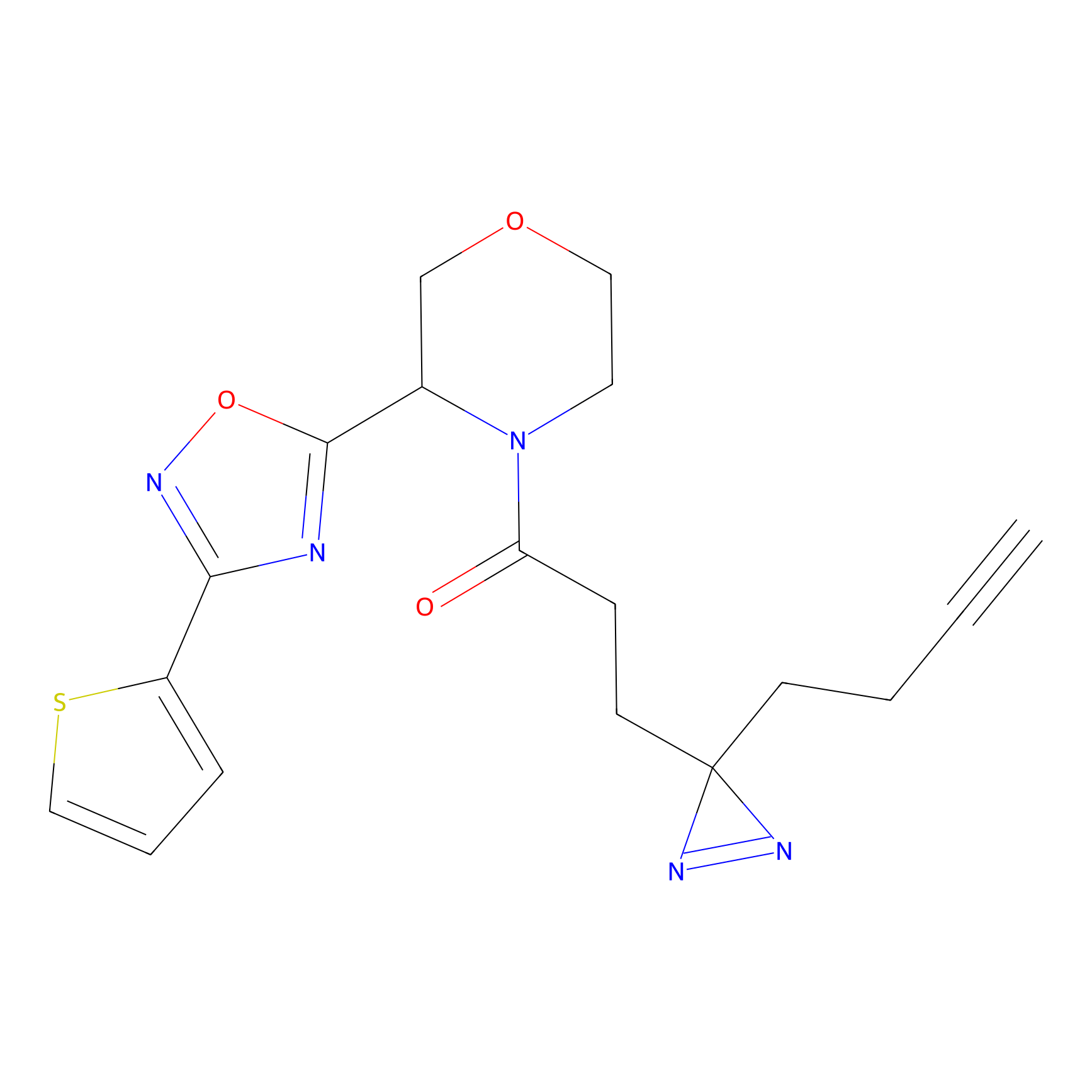
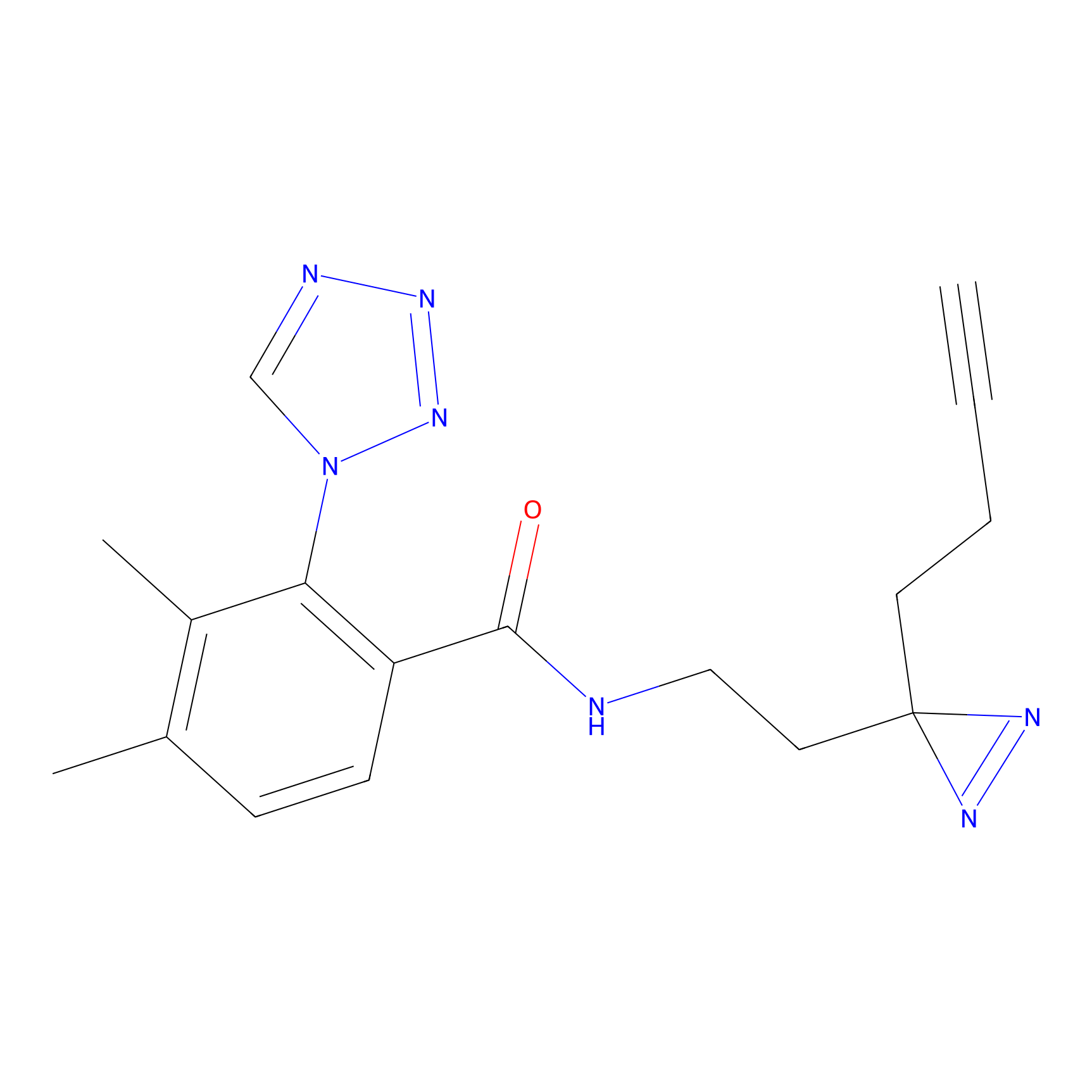
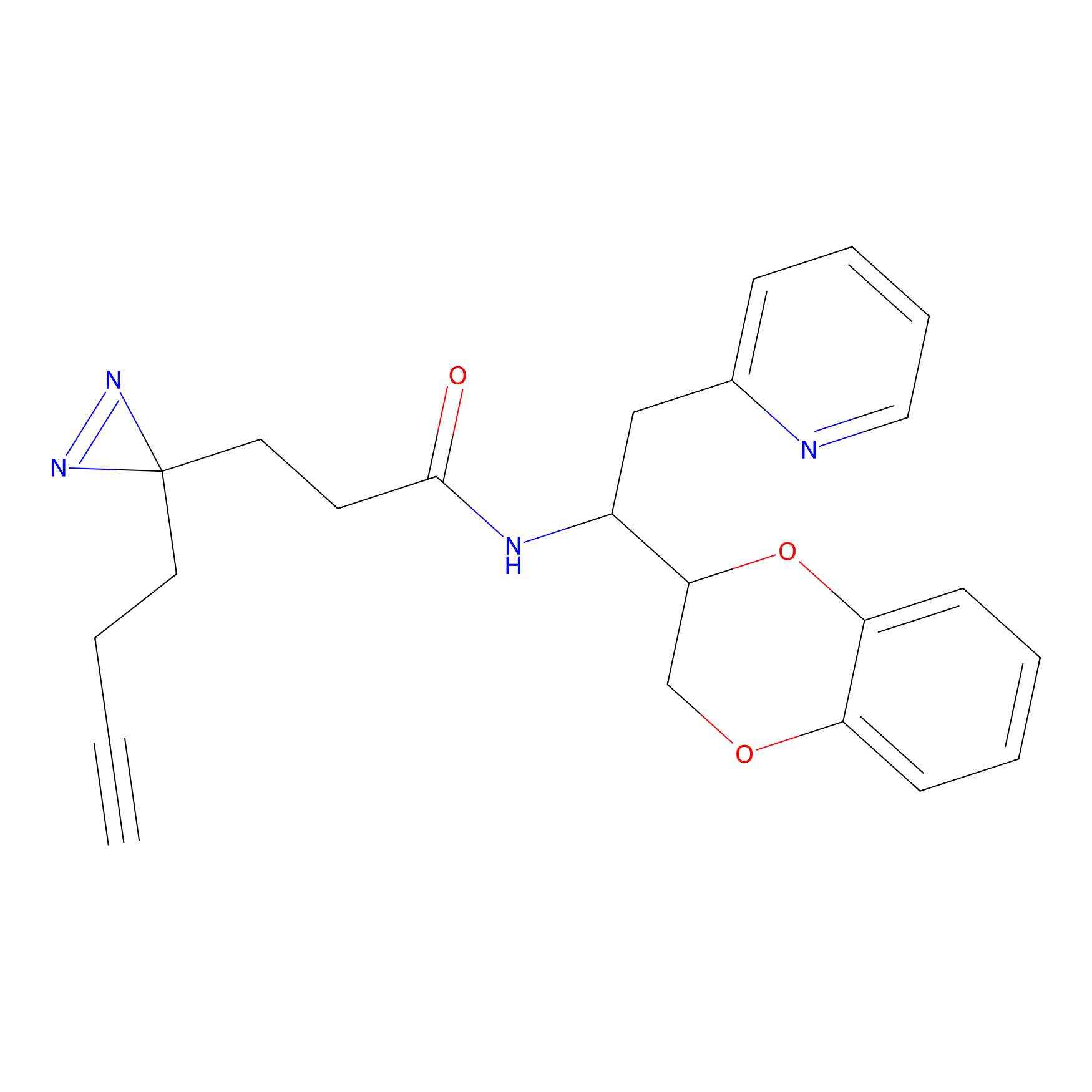
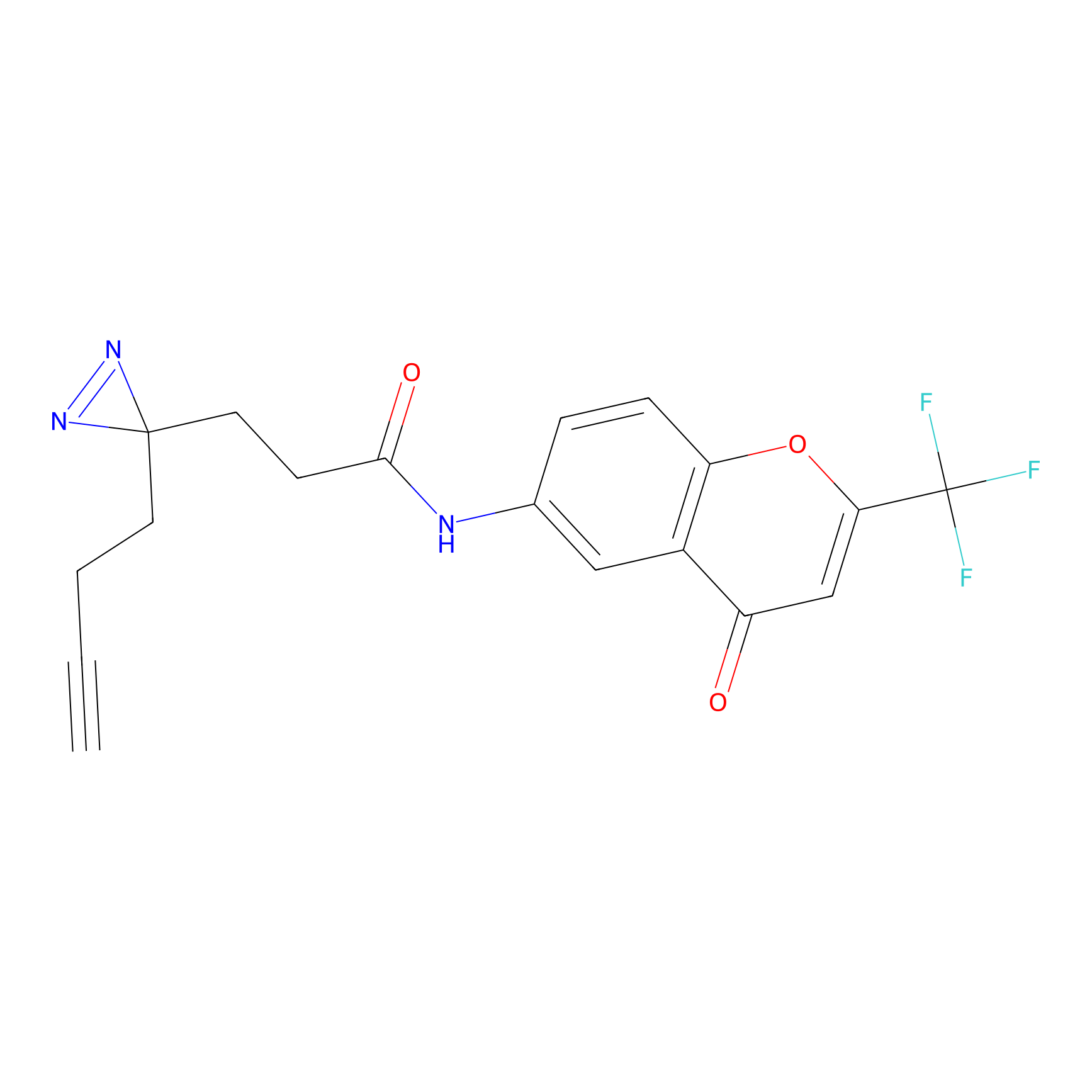
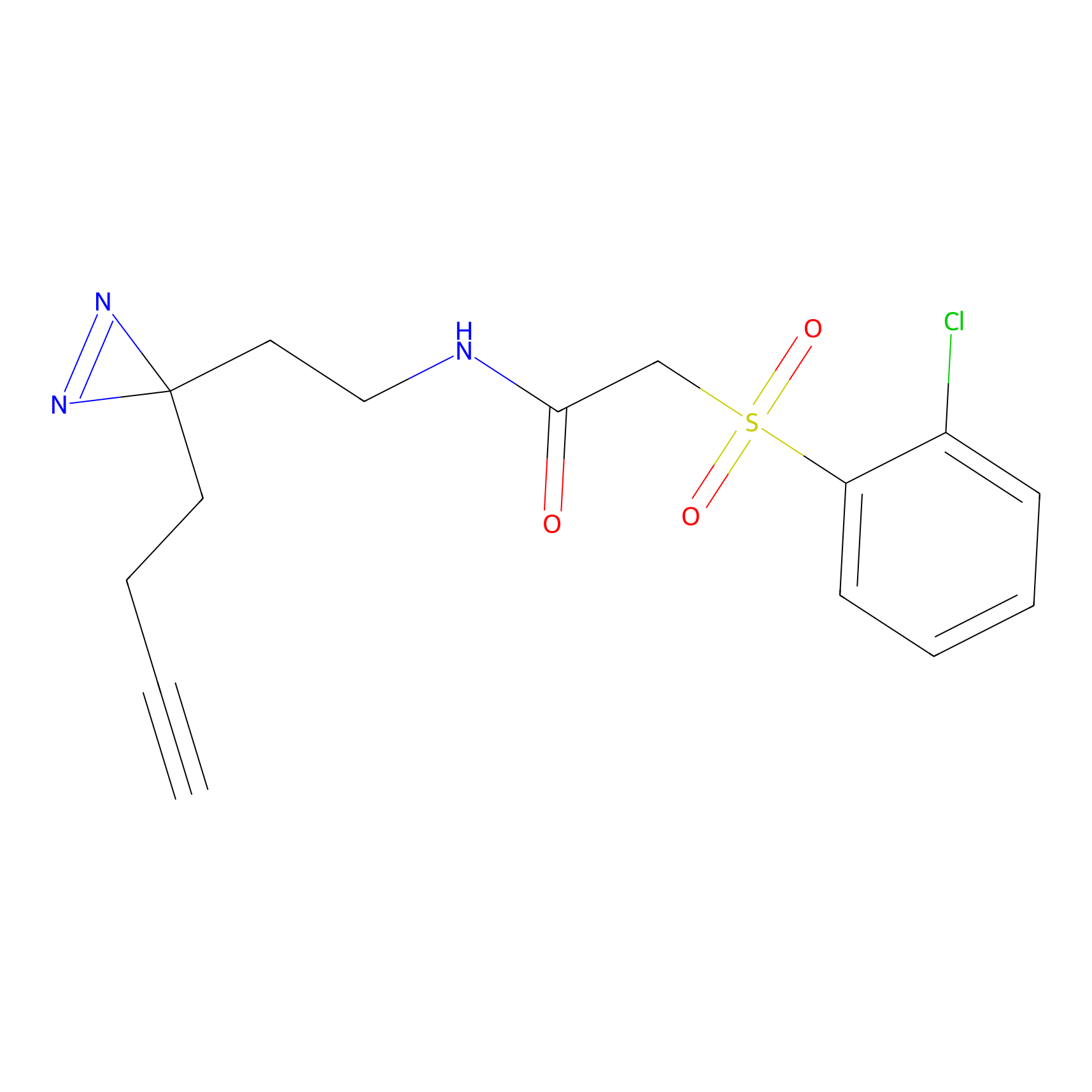
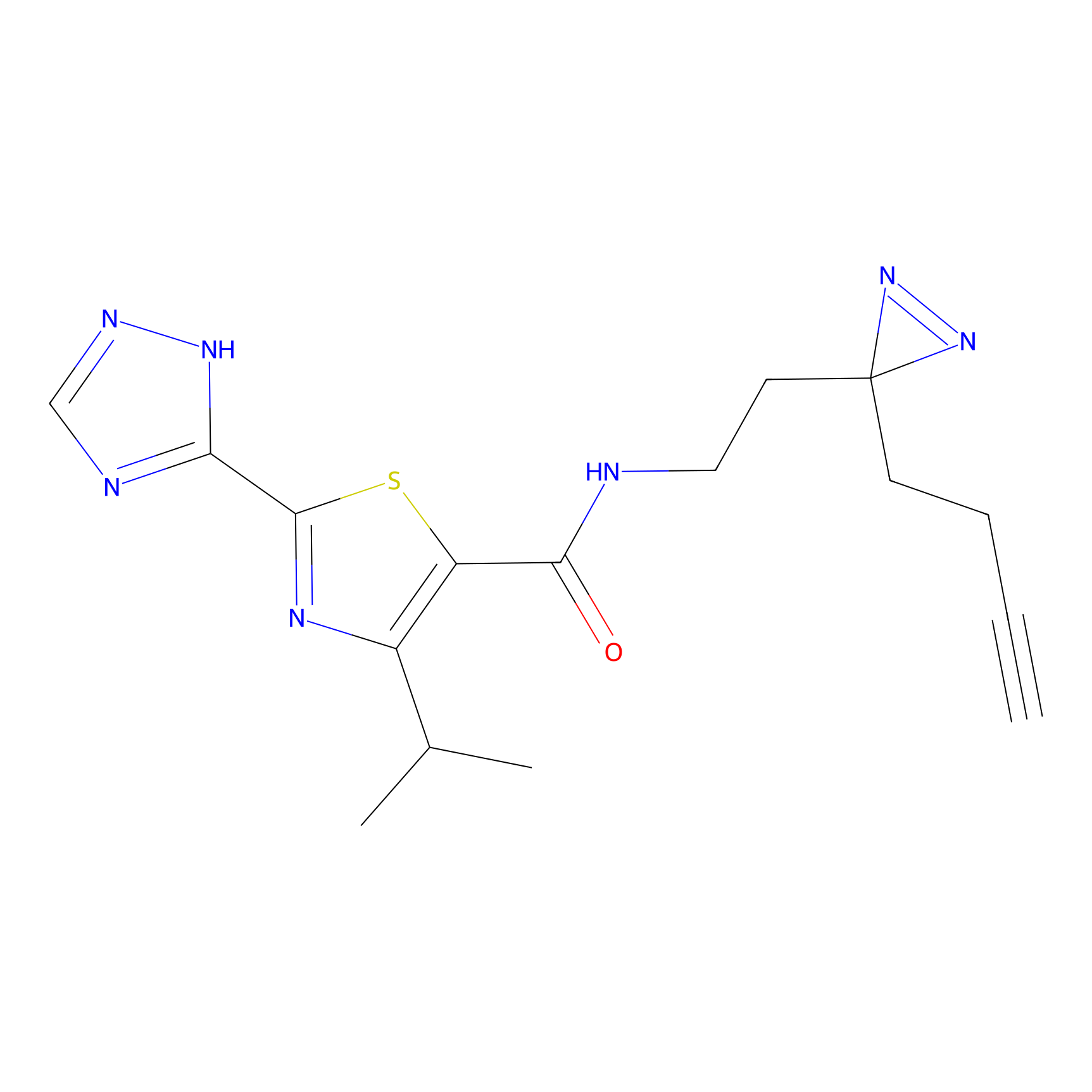
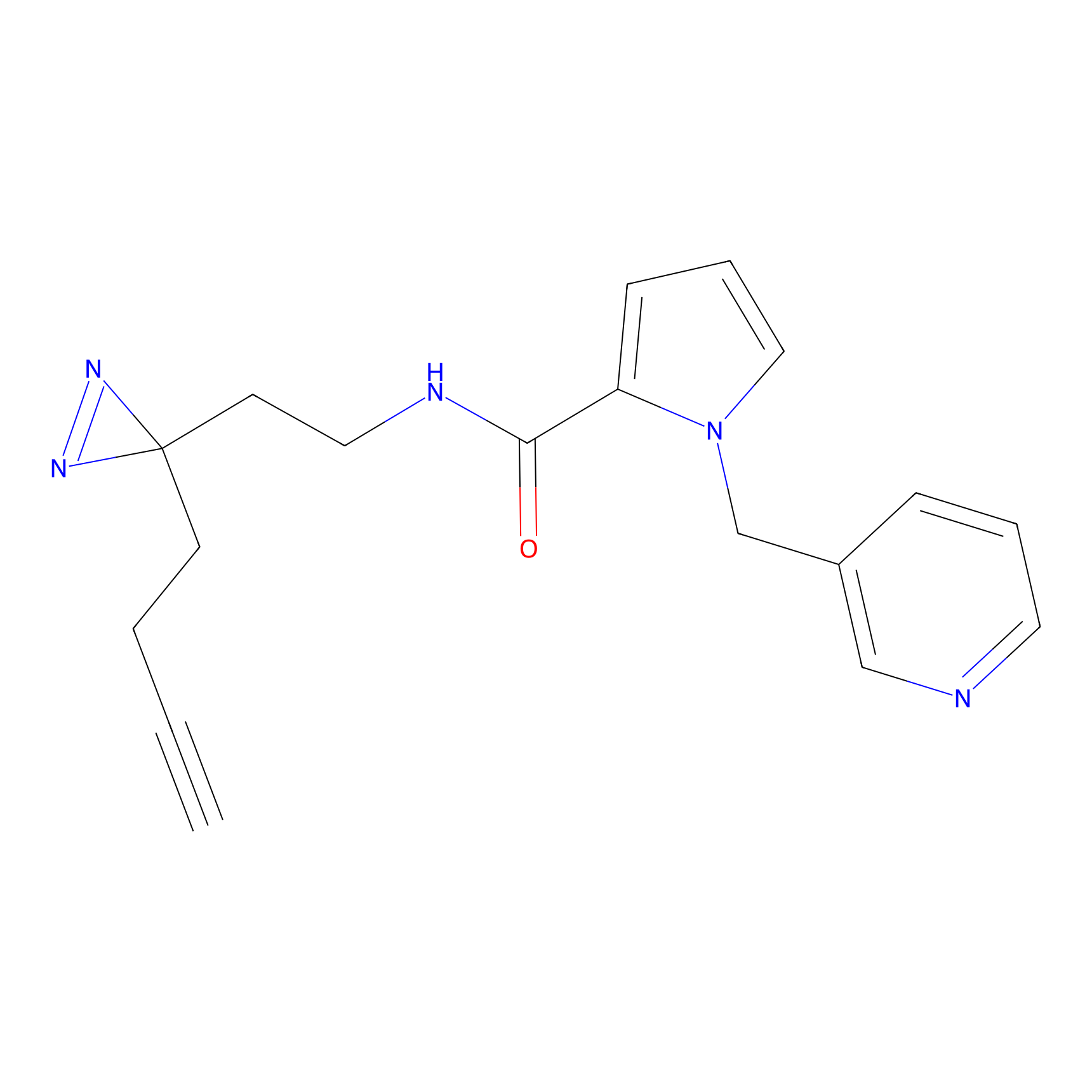
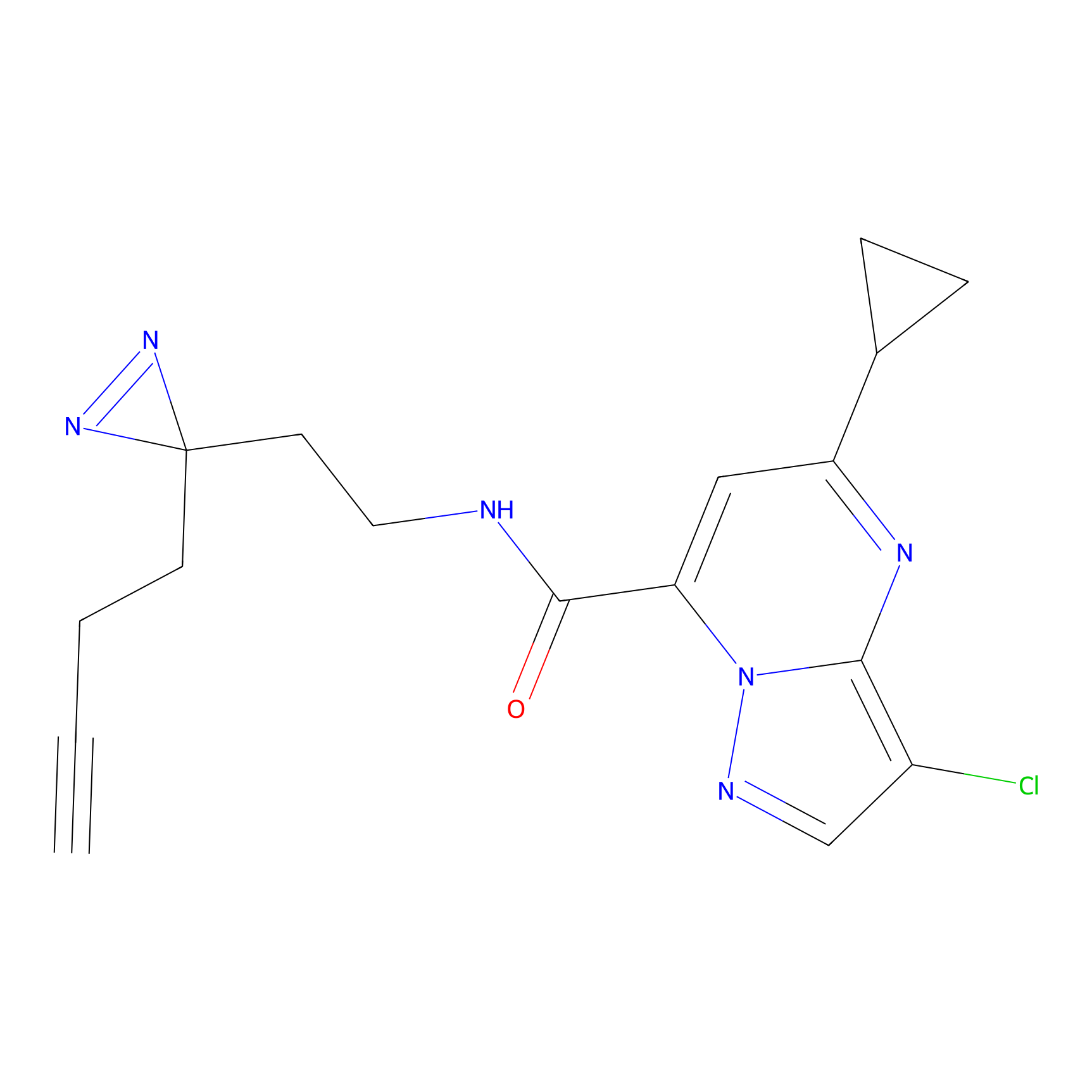
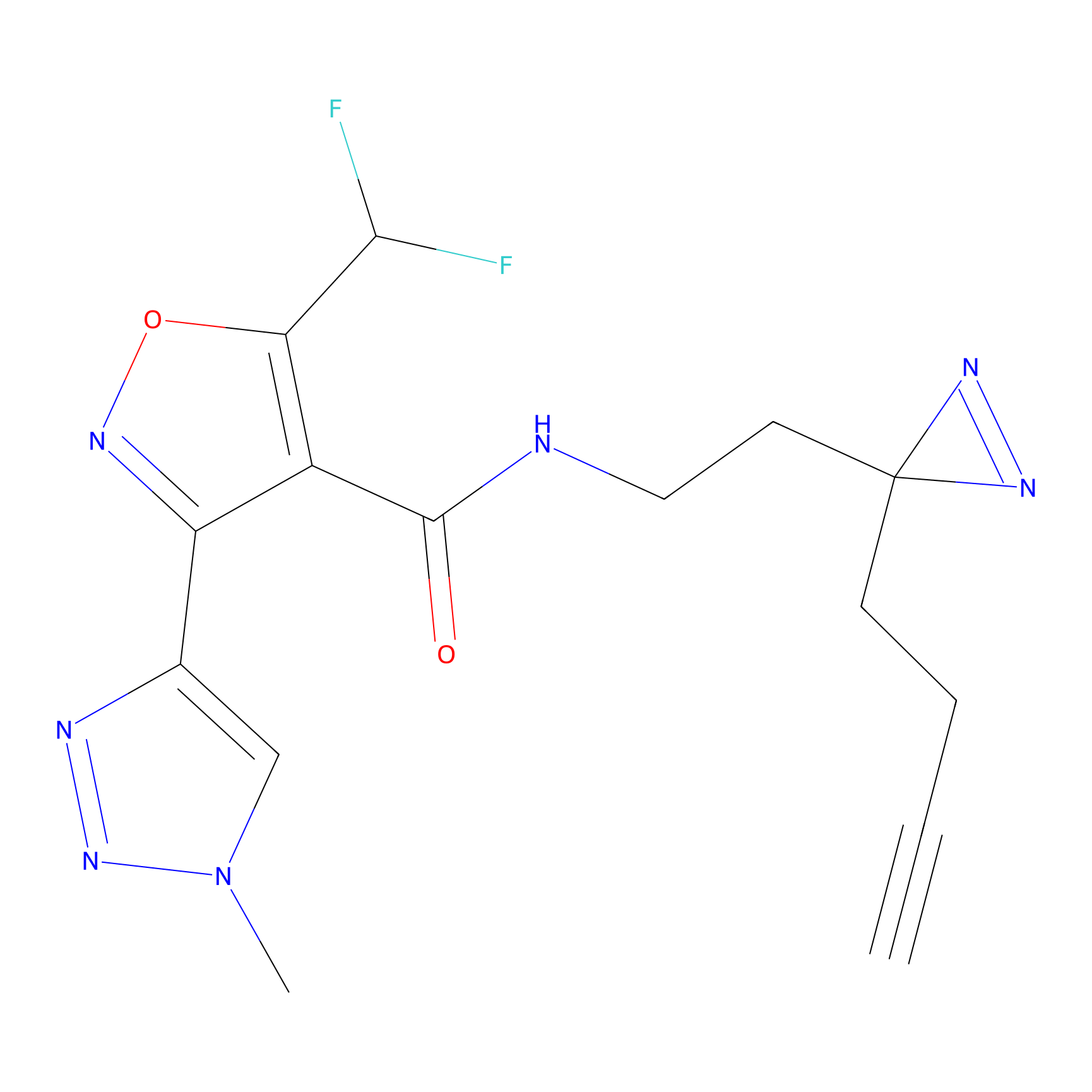
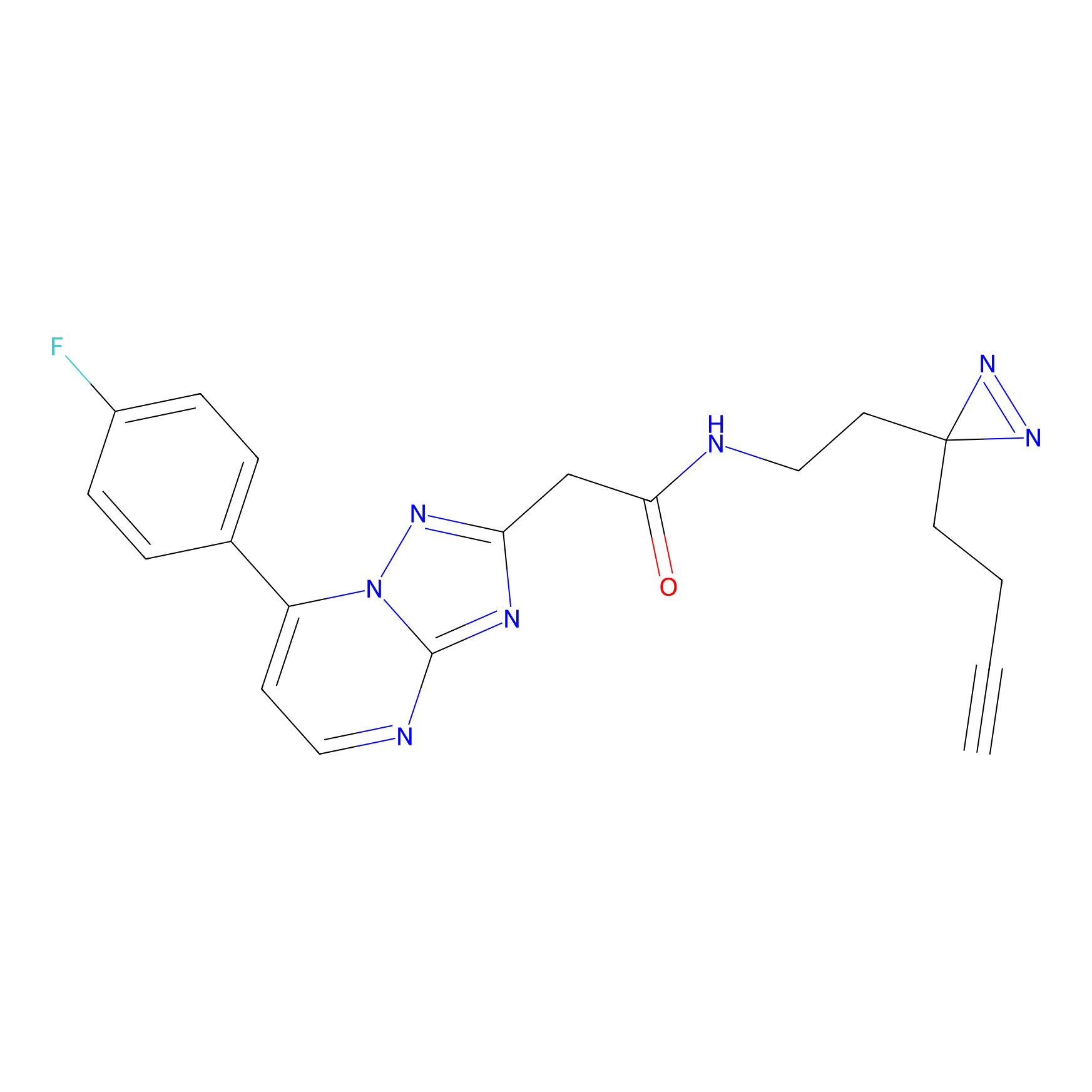
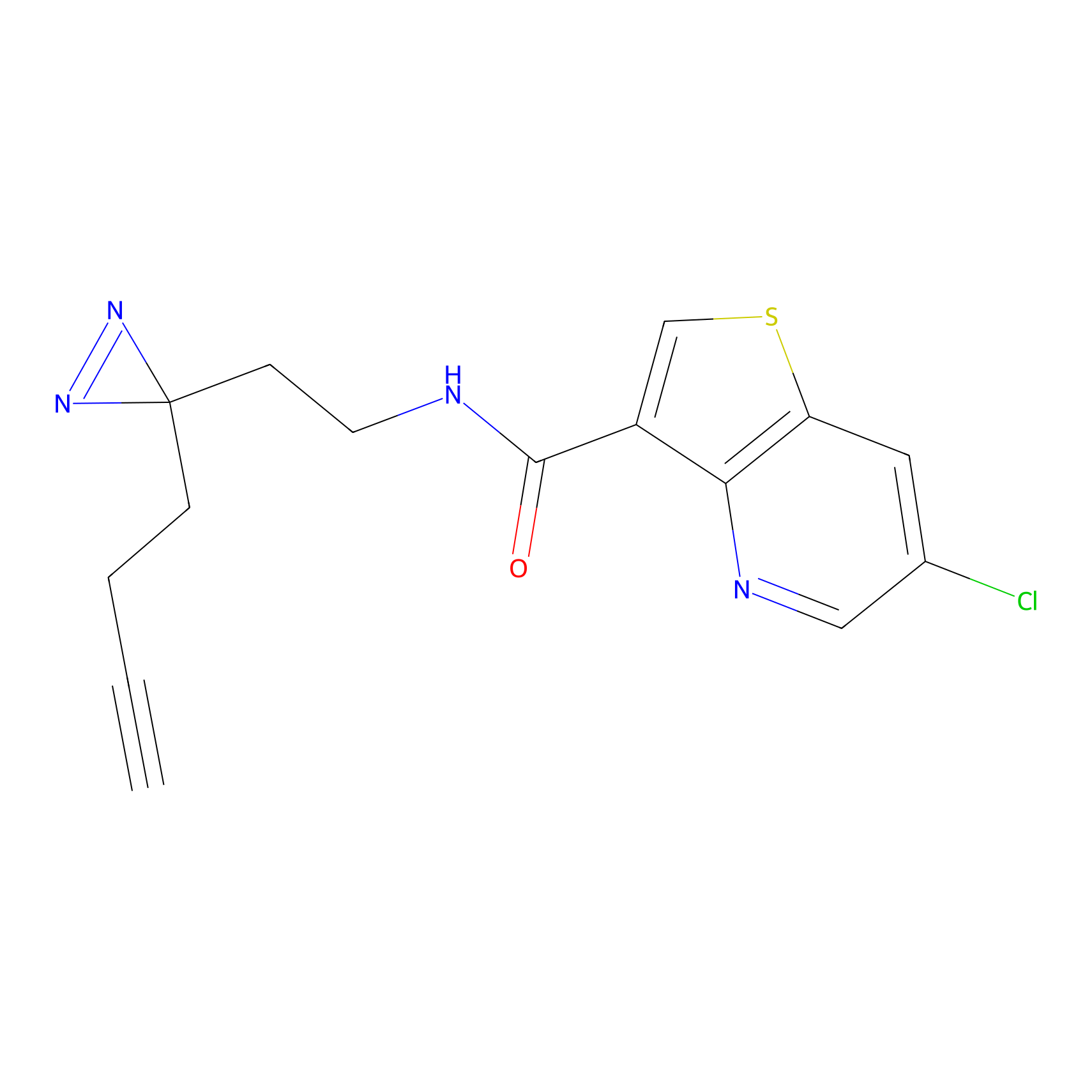
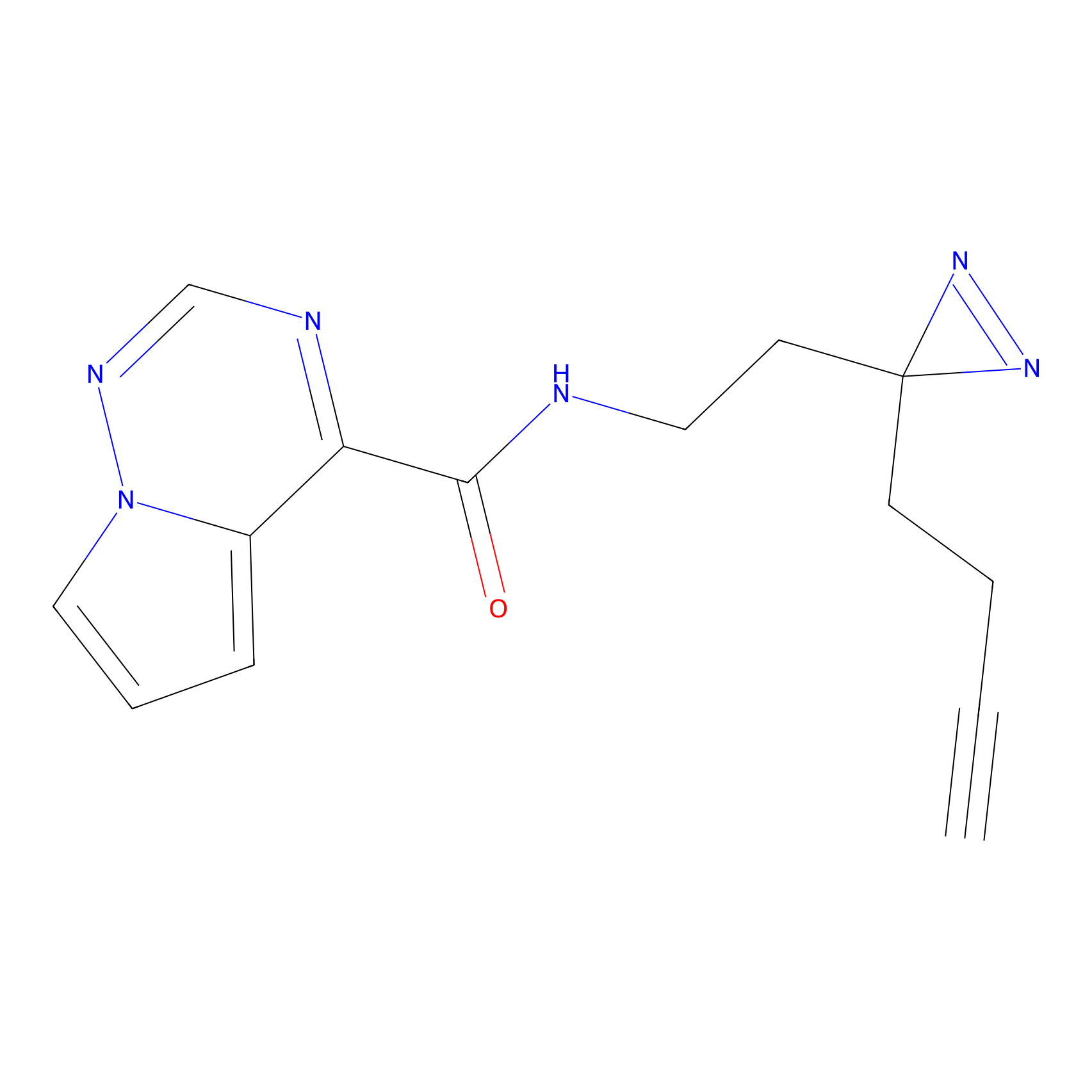
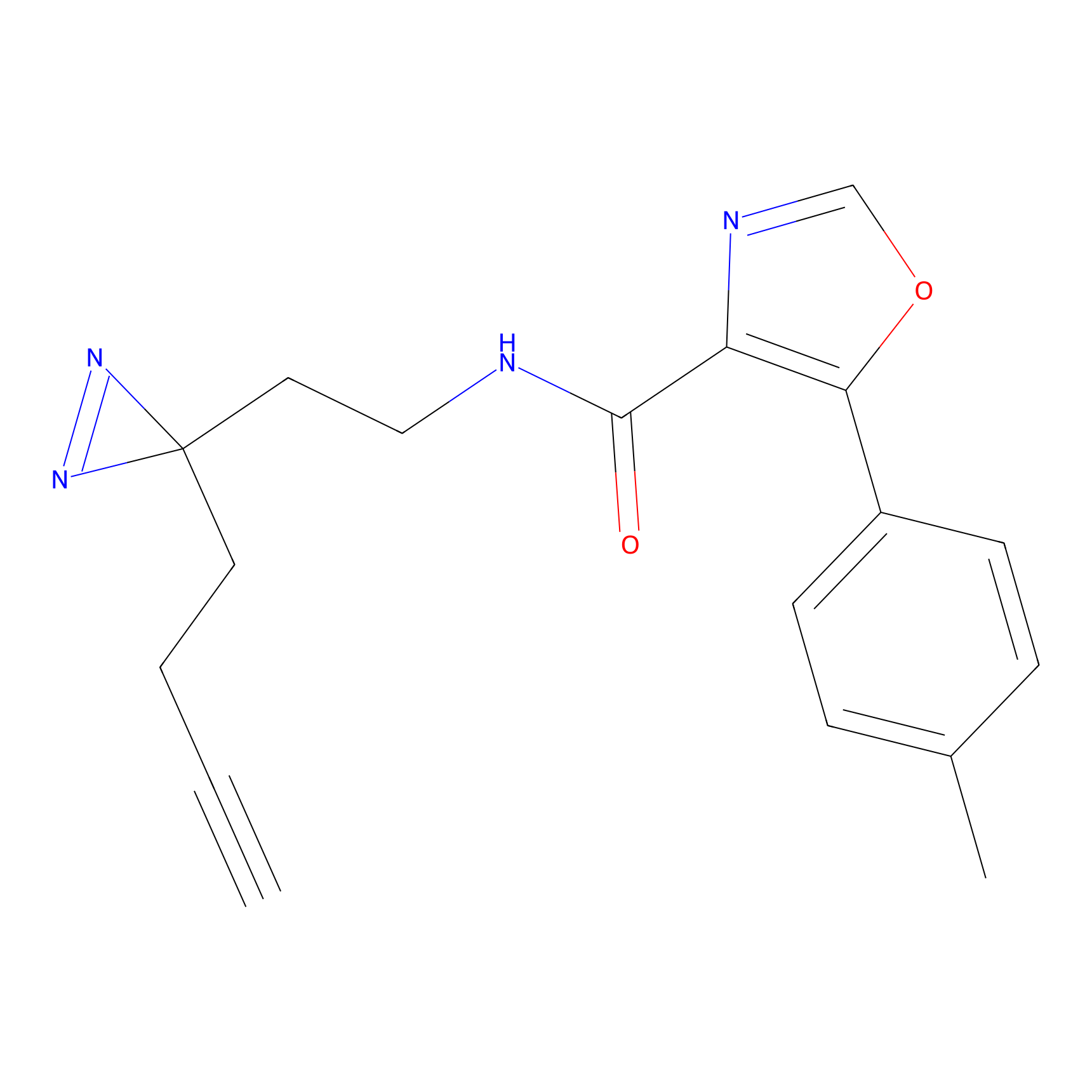
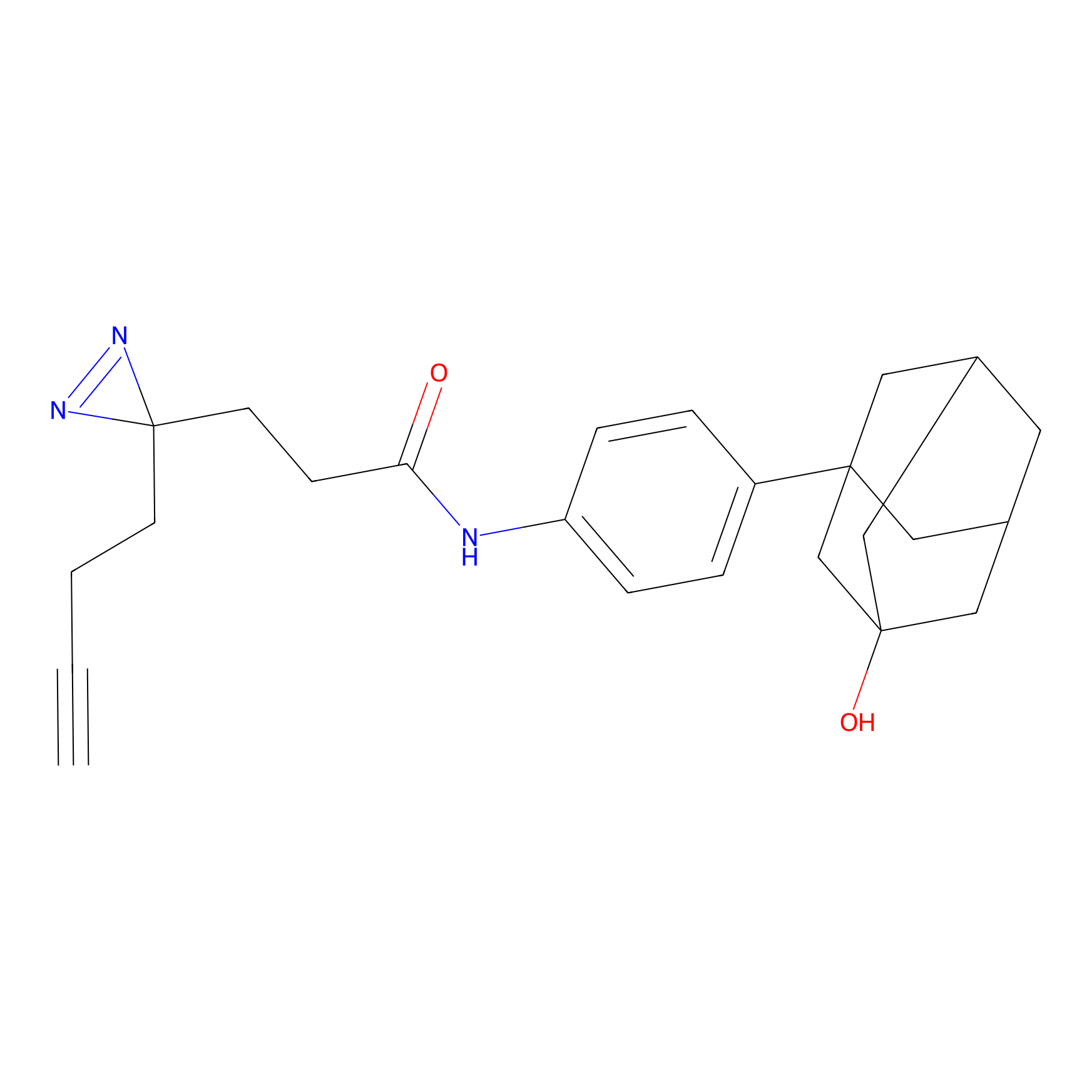
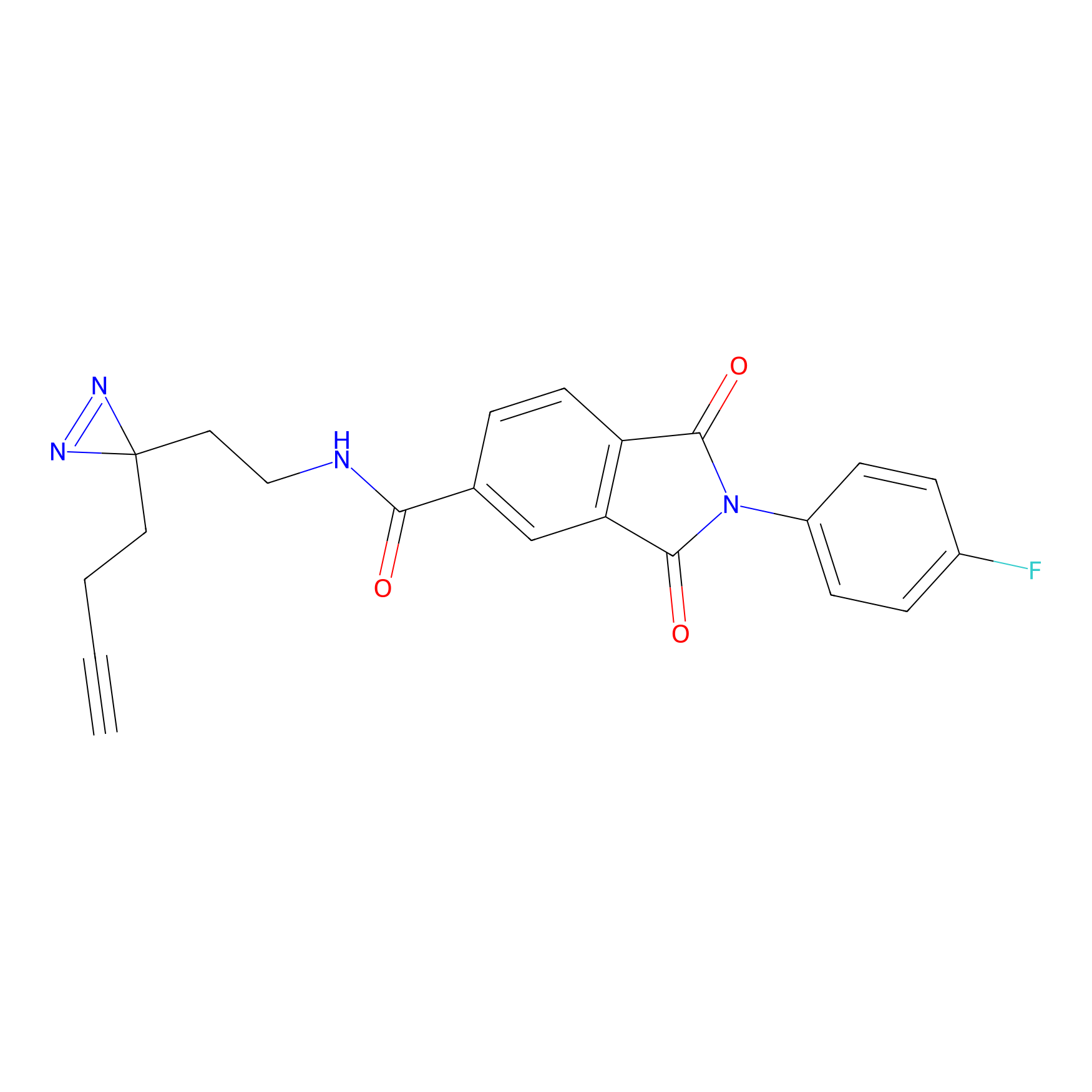
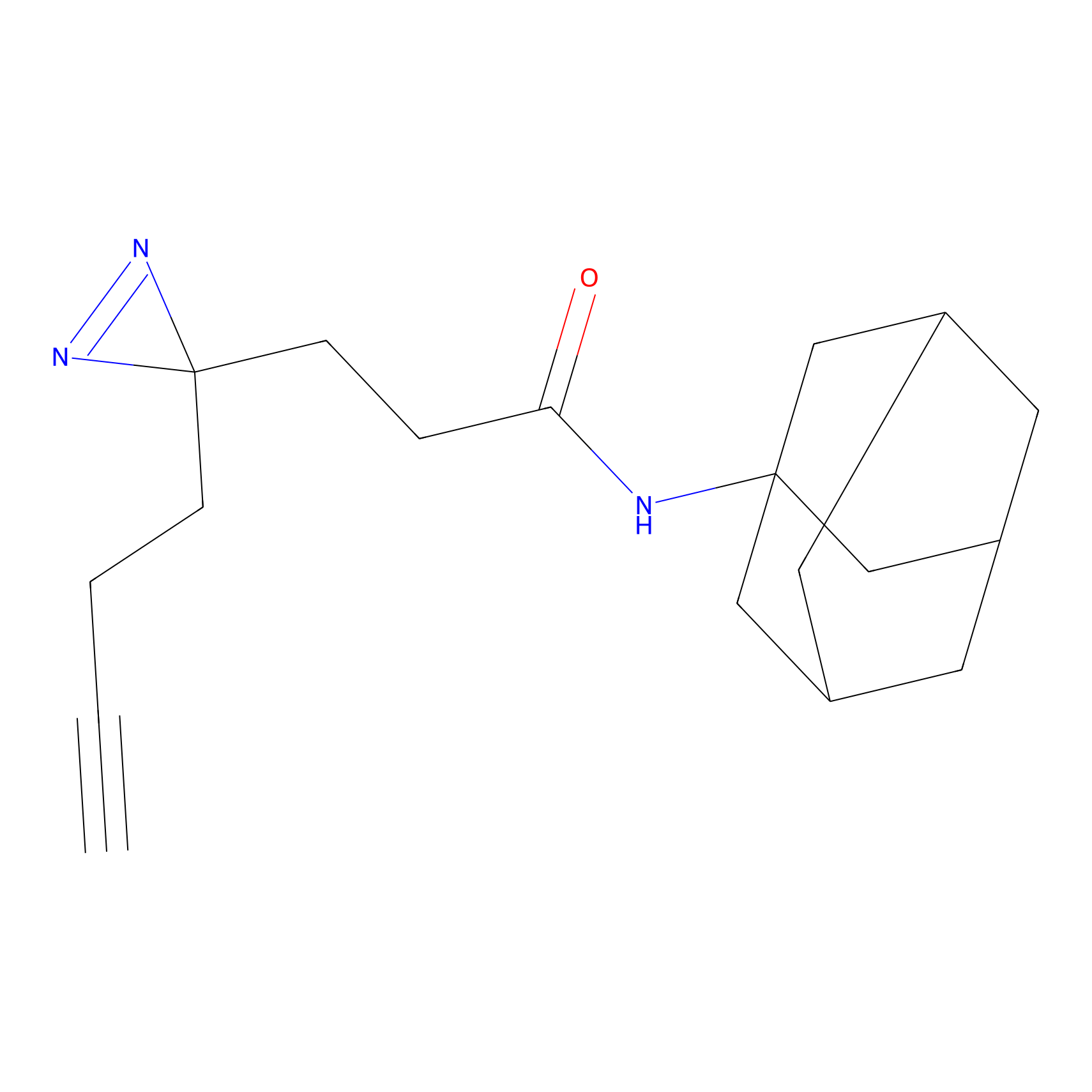
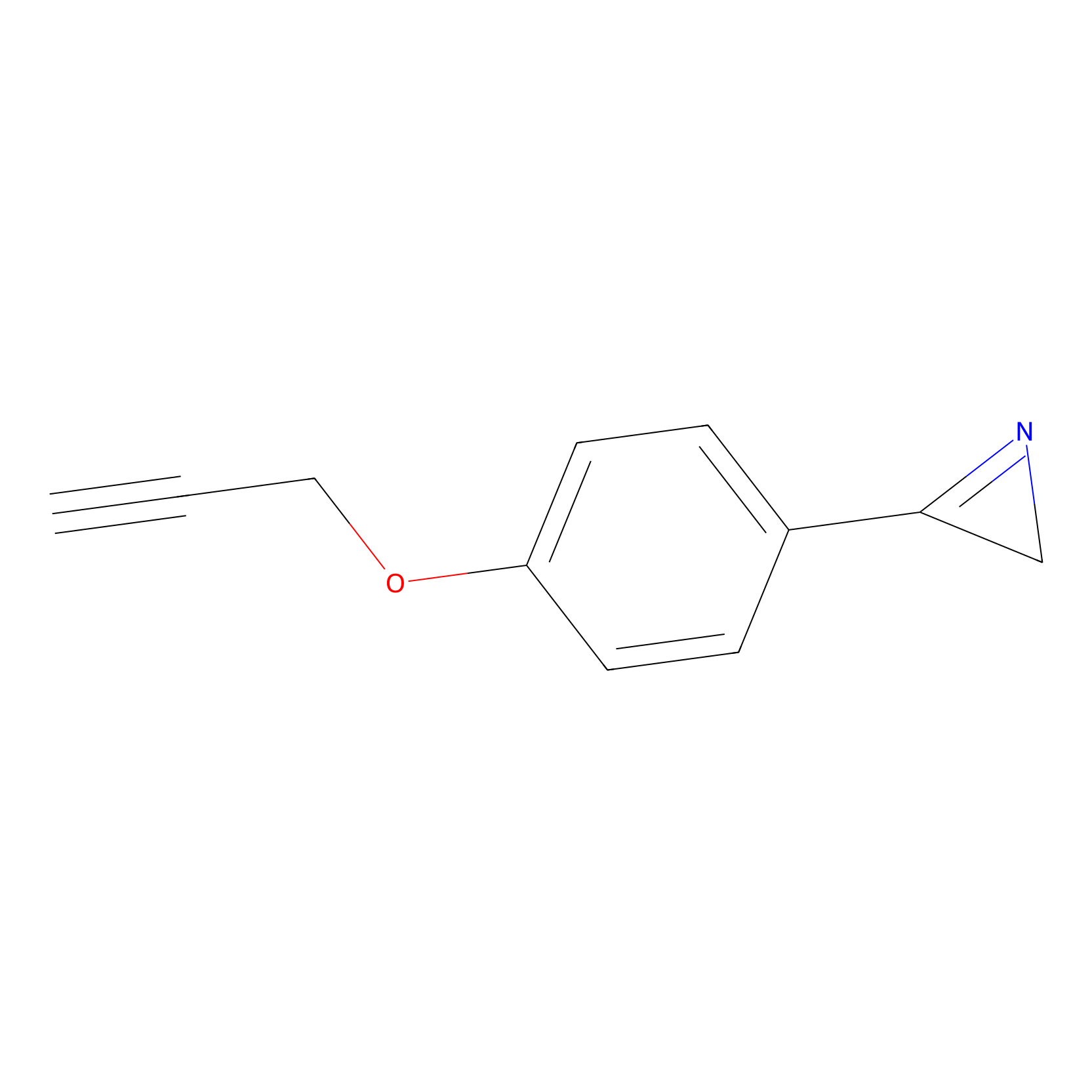
|
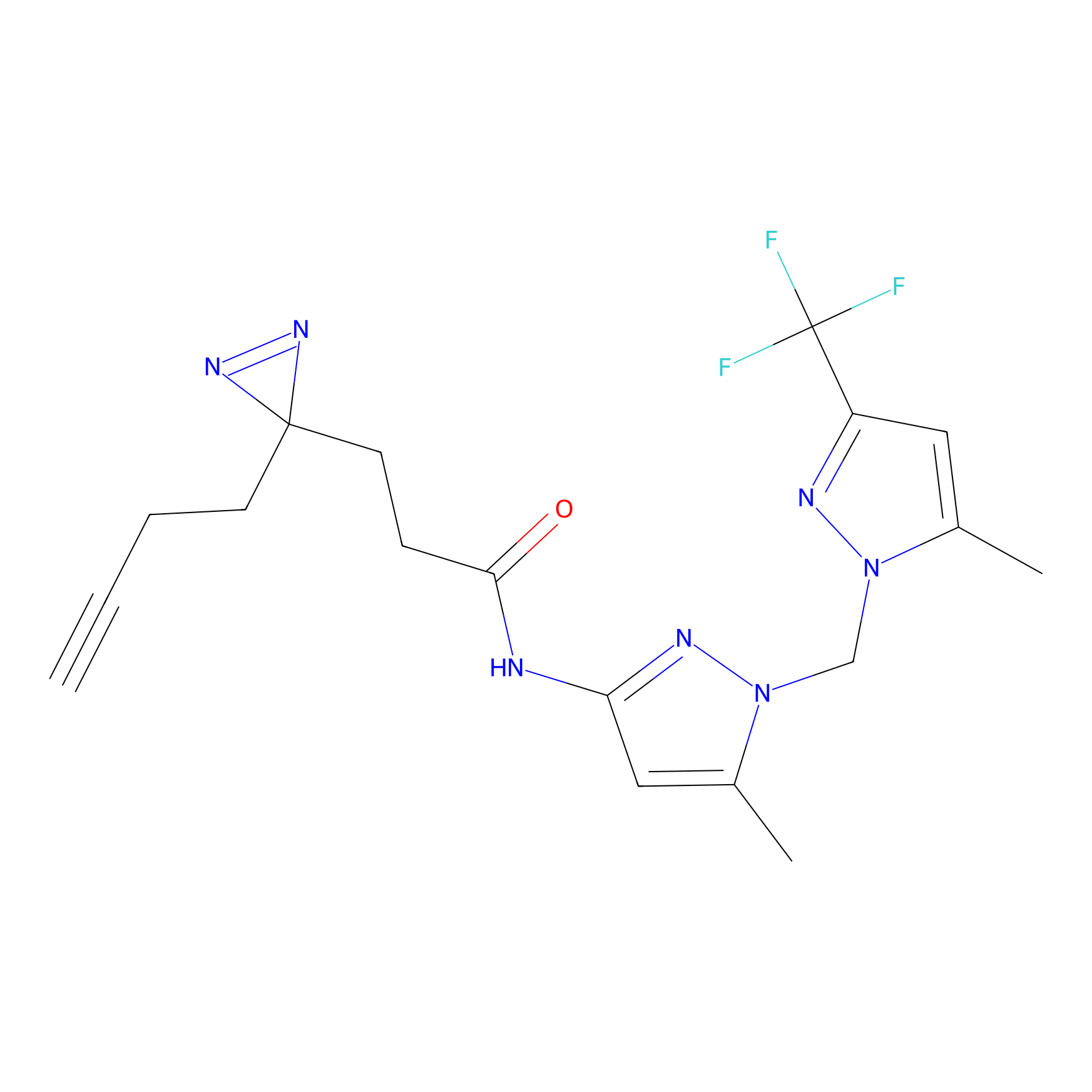
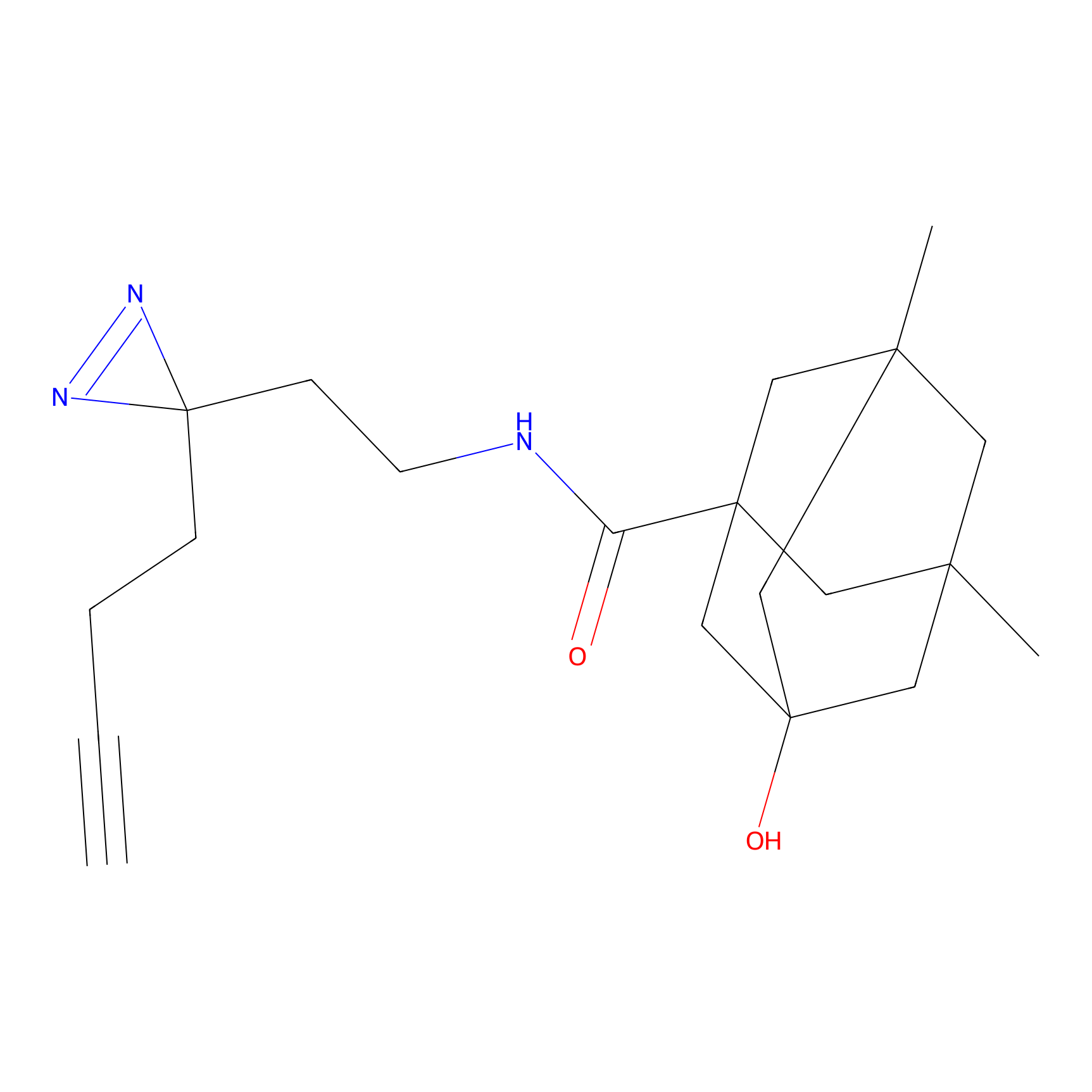
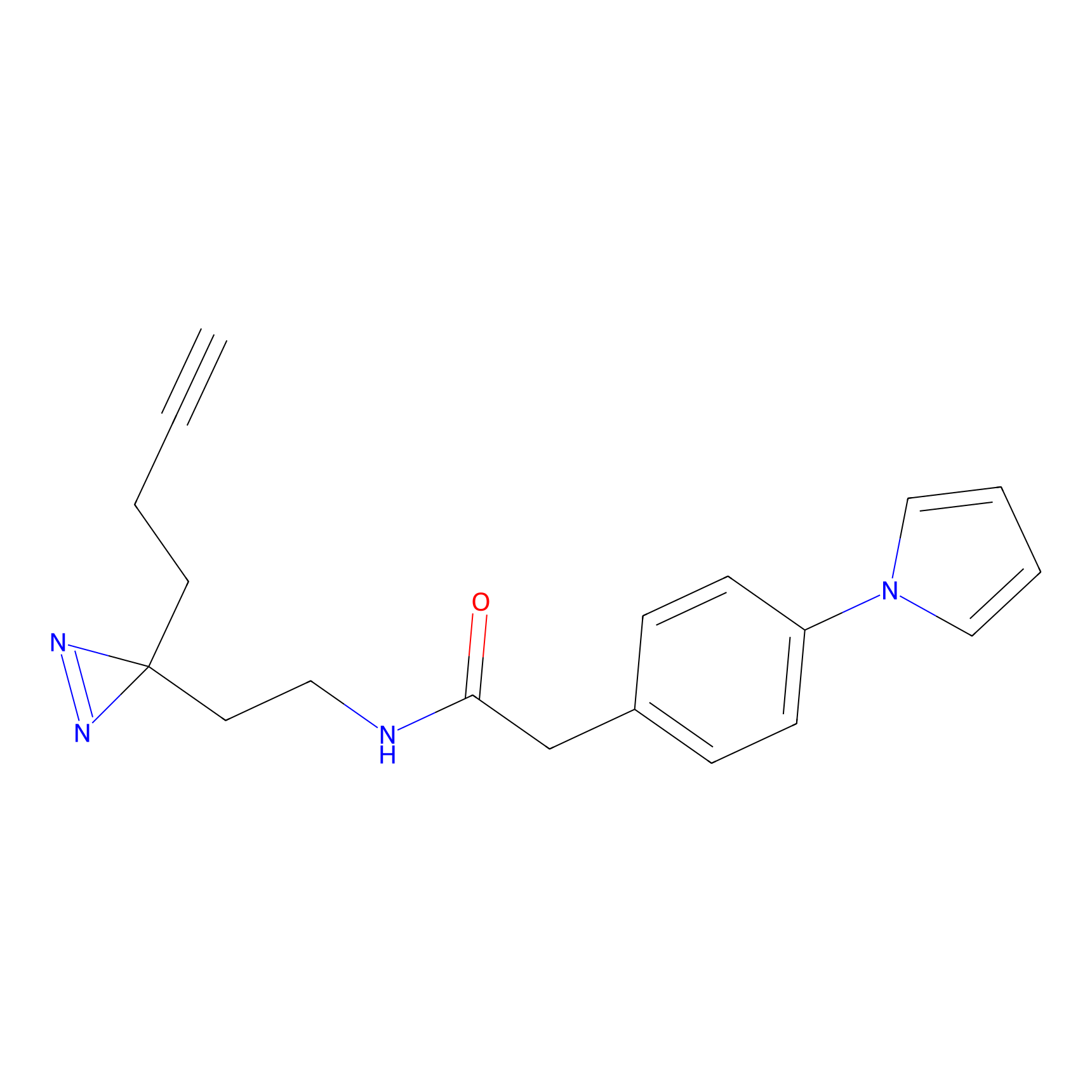
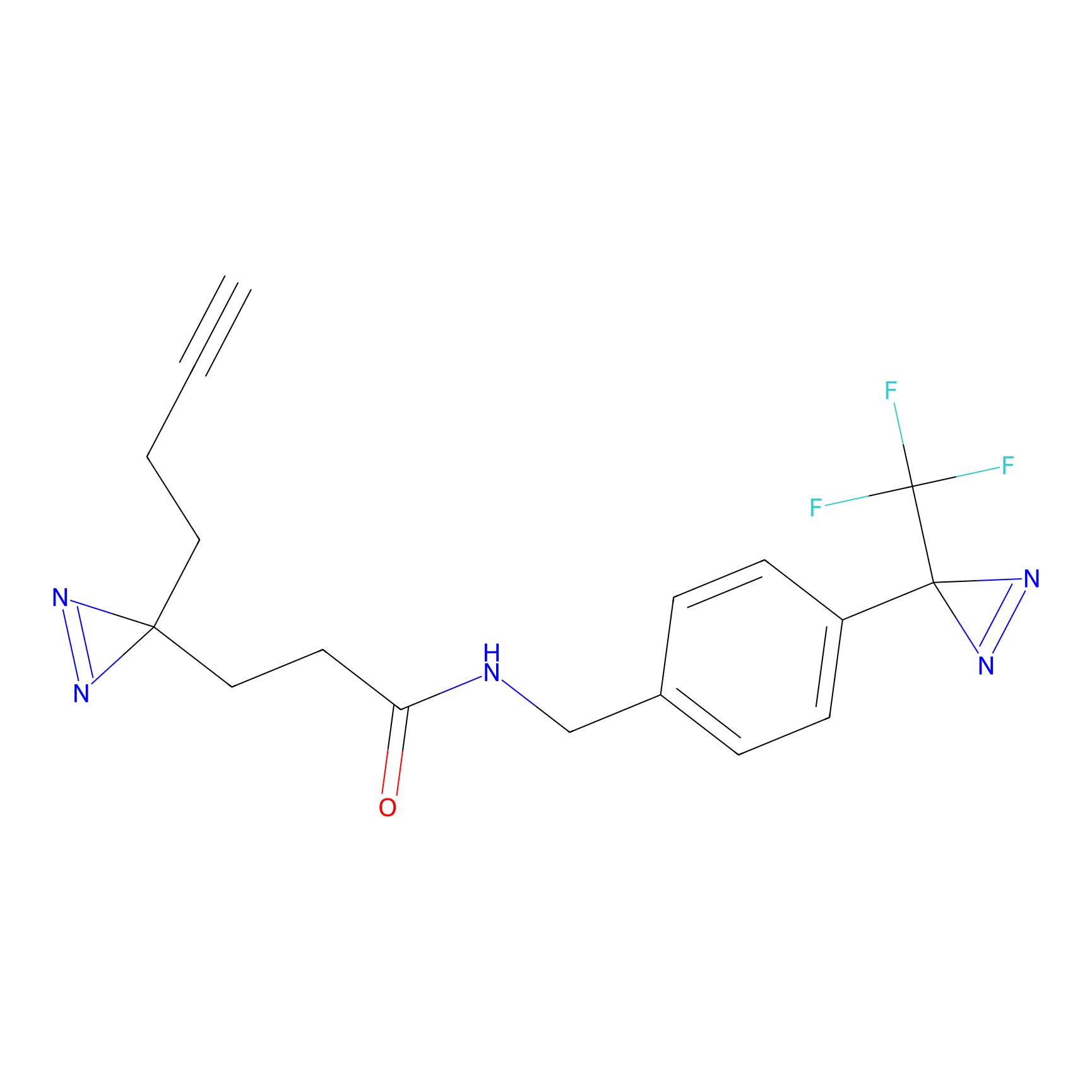
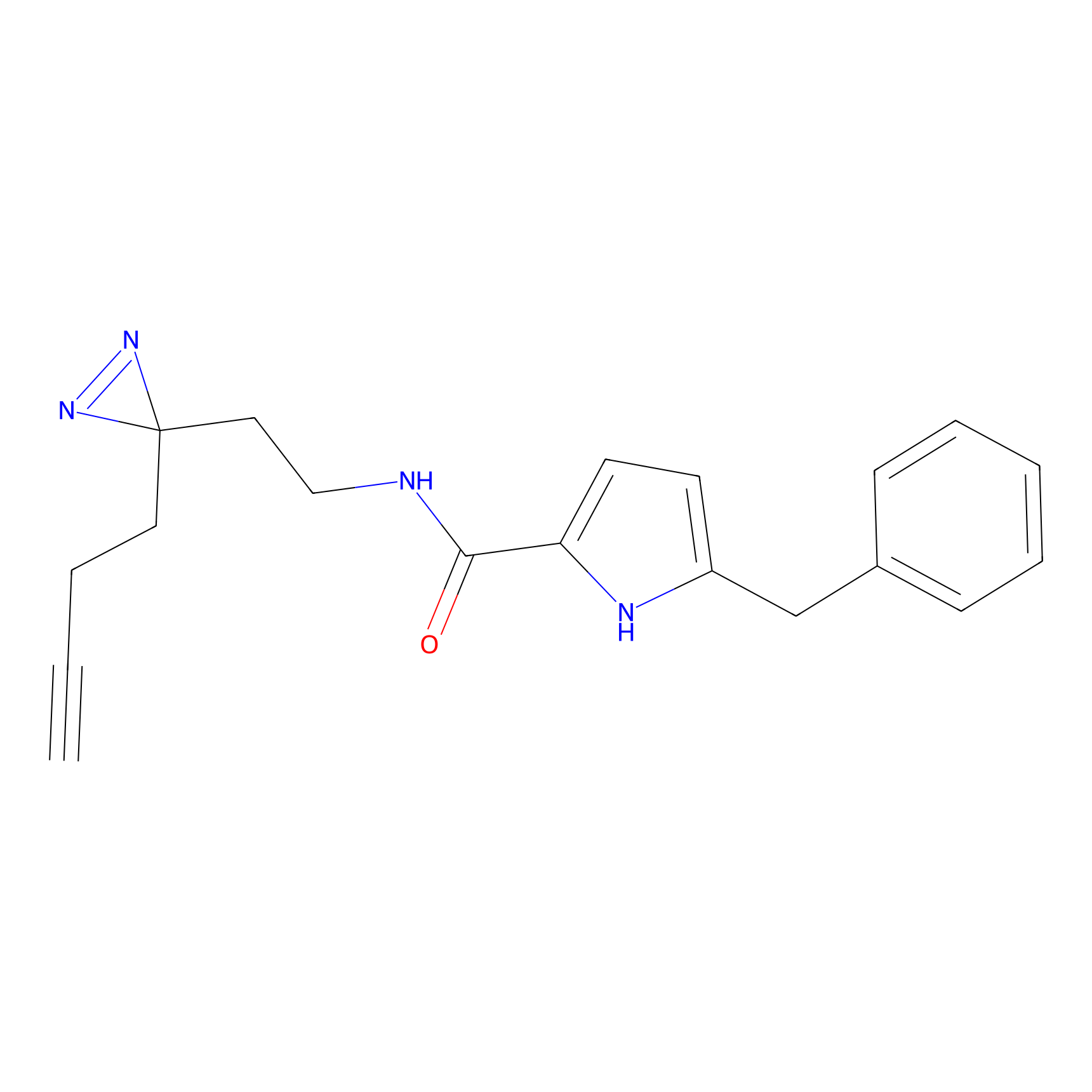
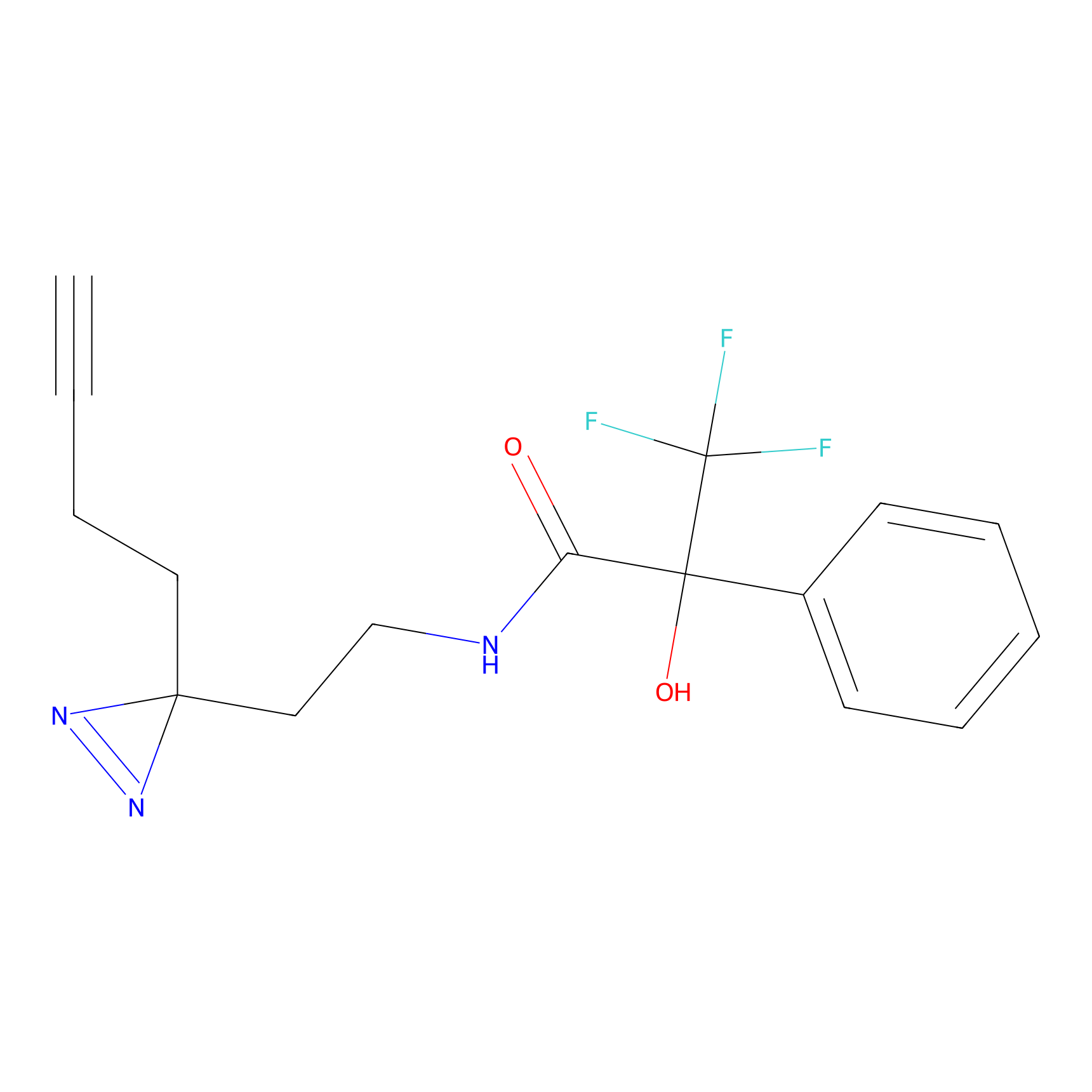
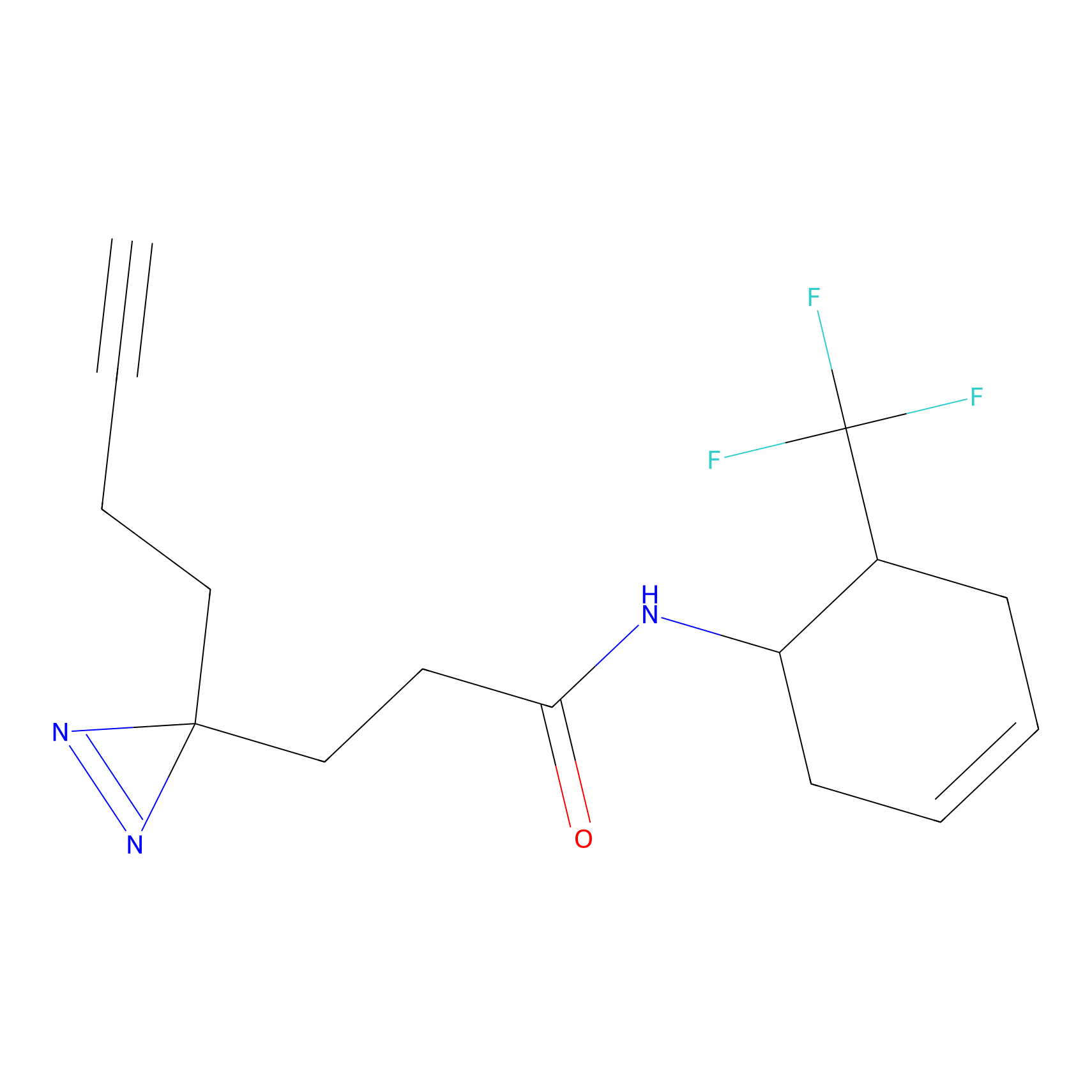
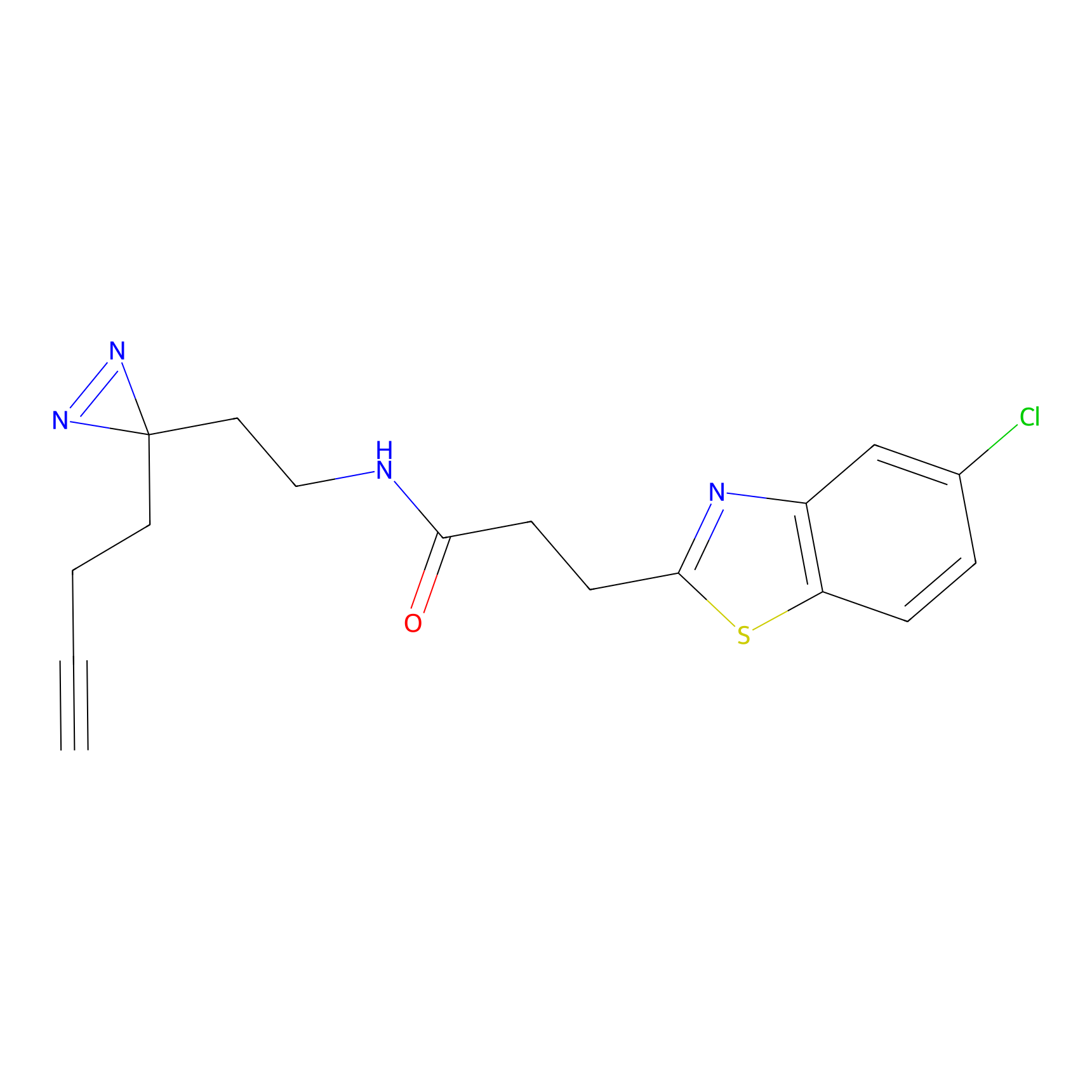
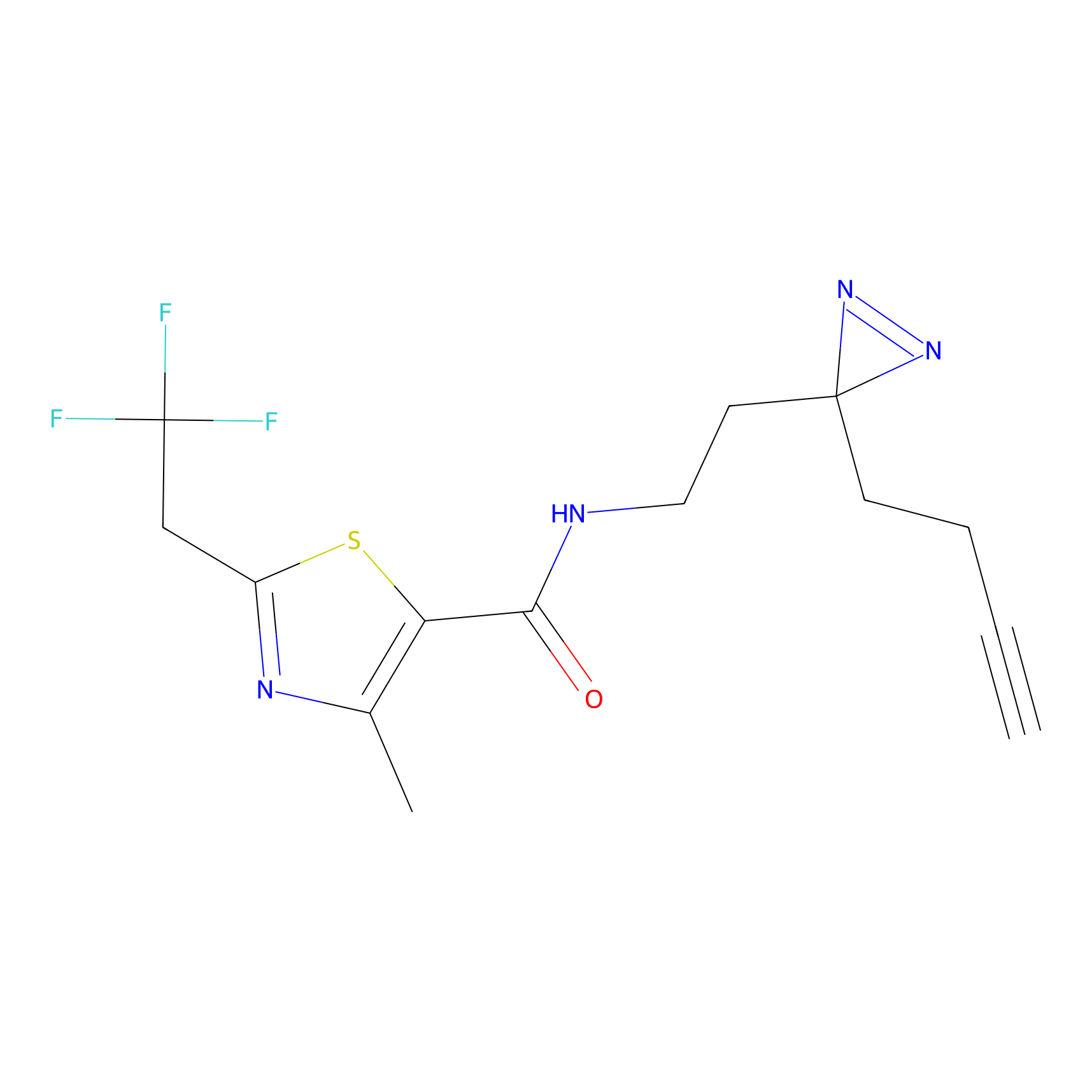
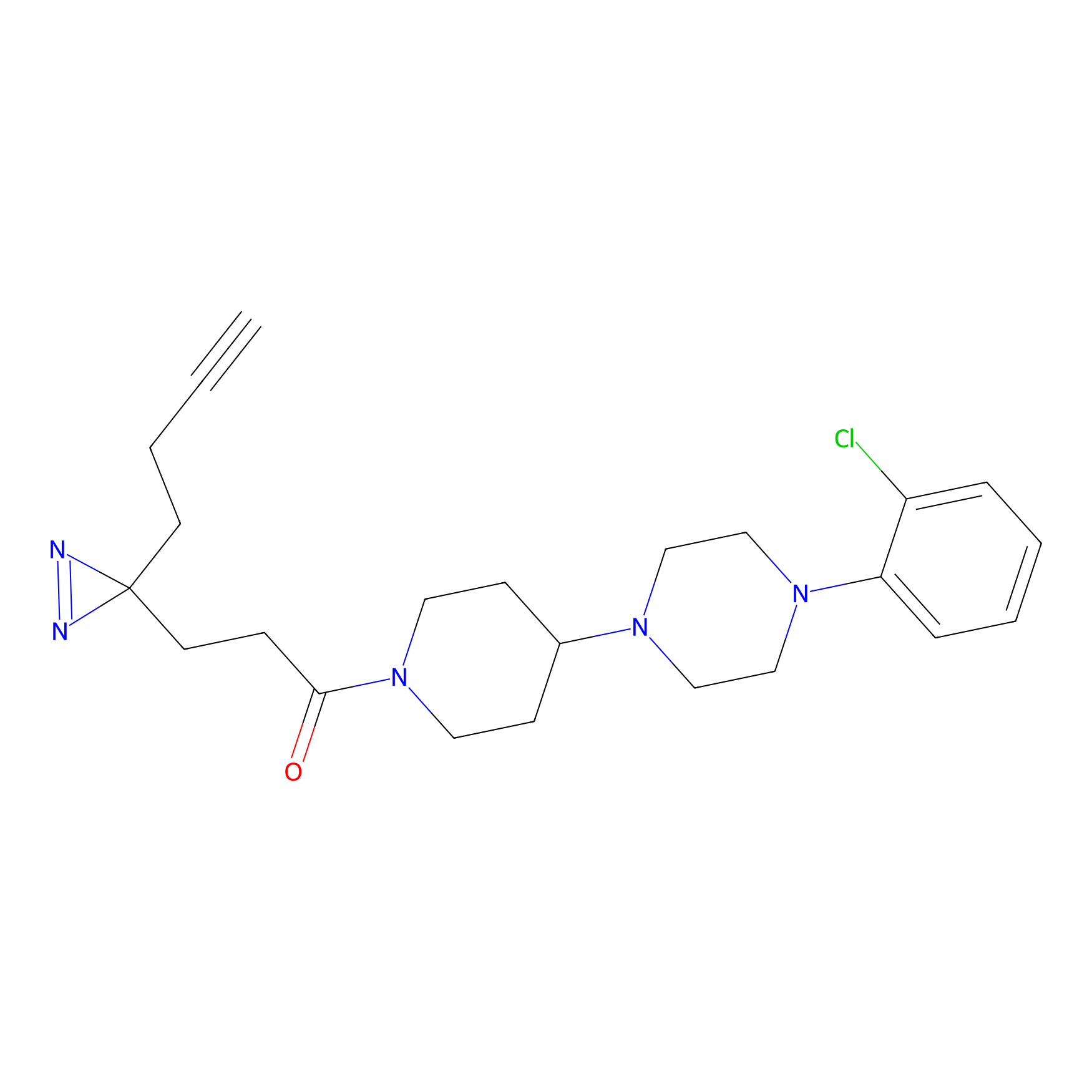
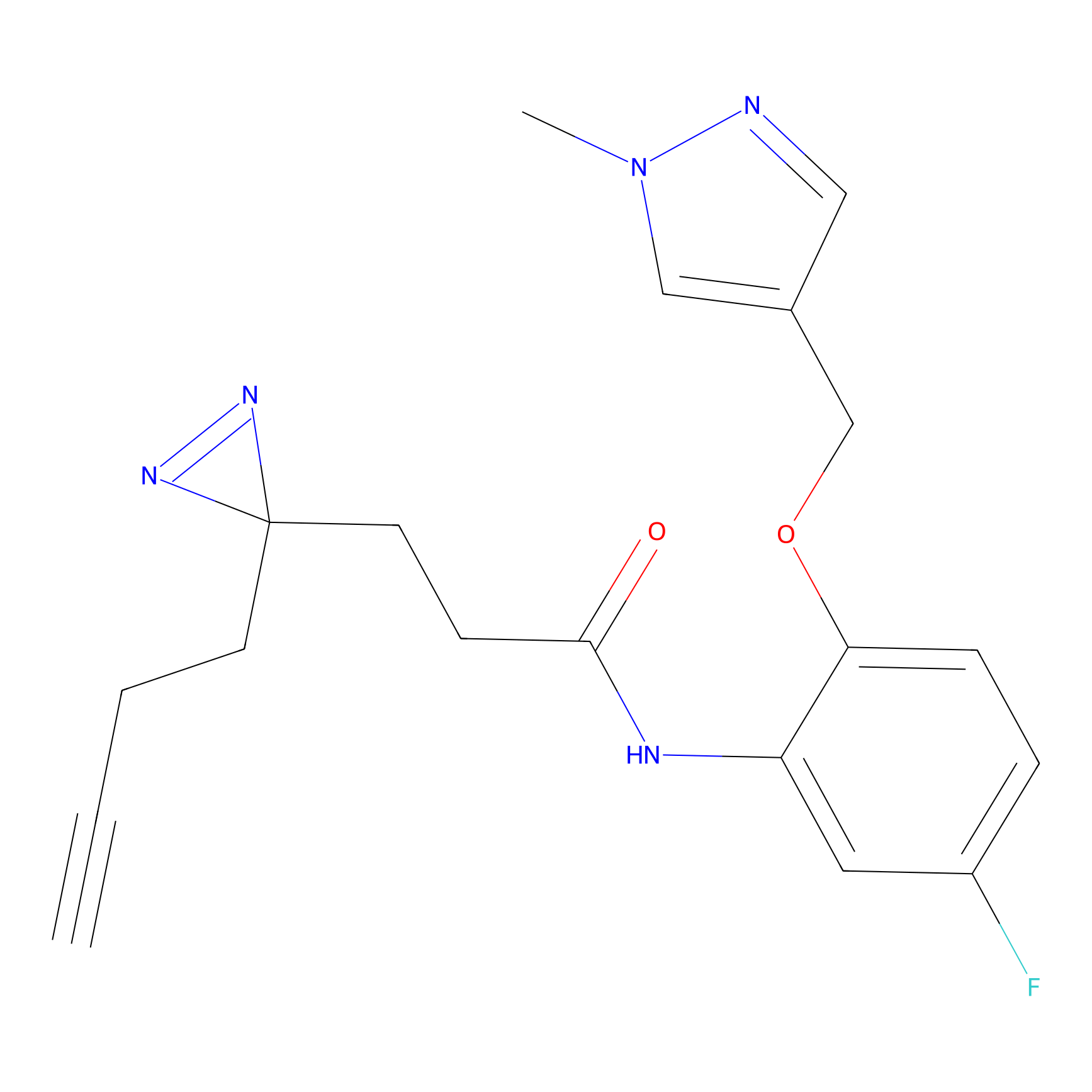
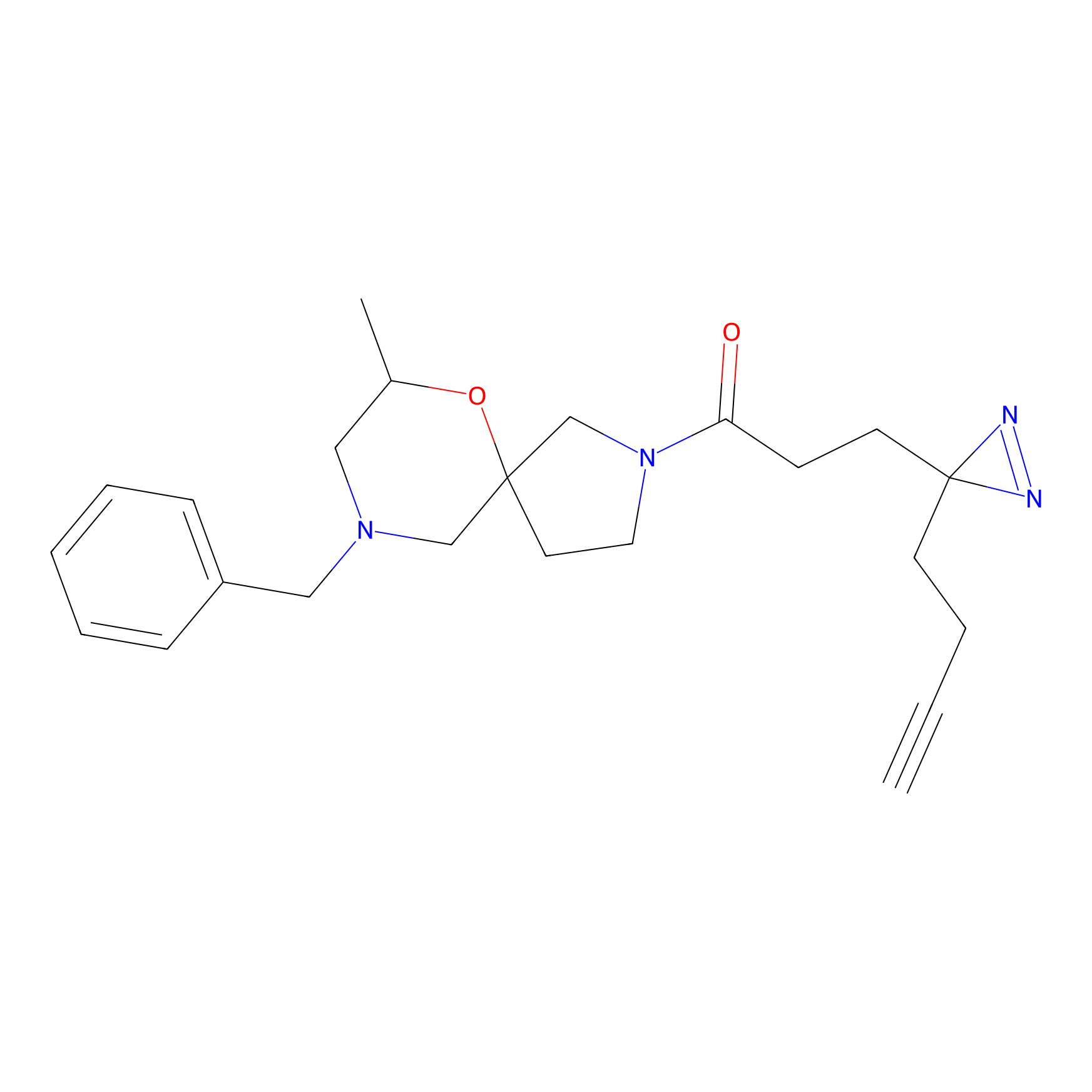
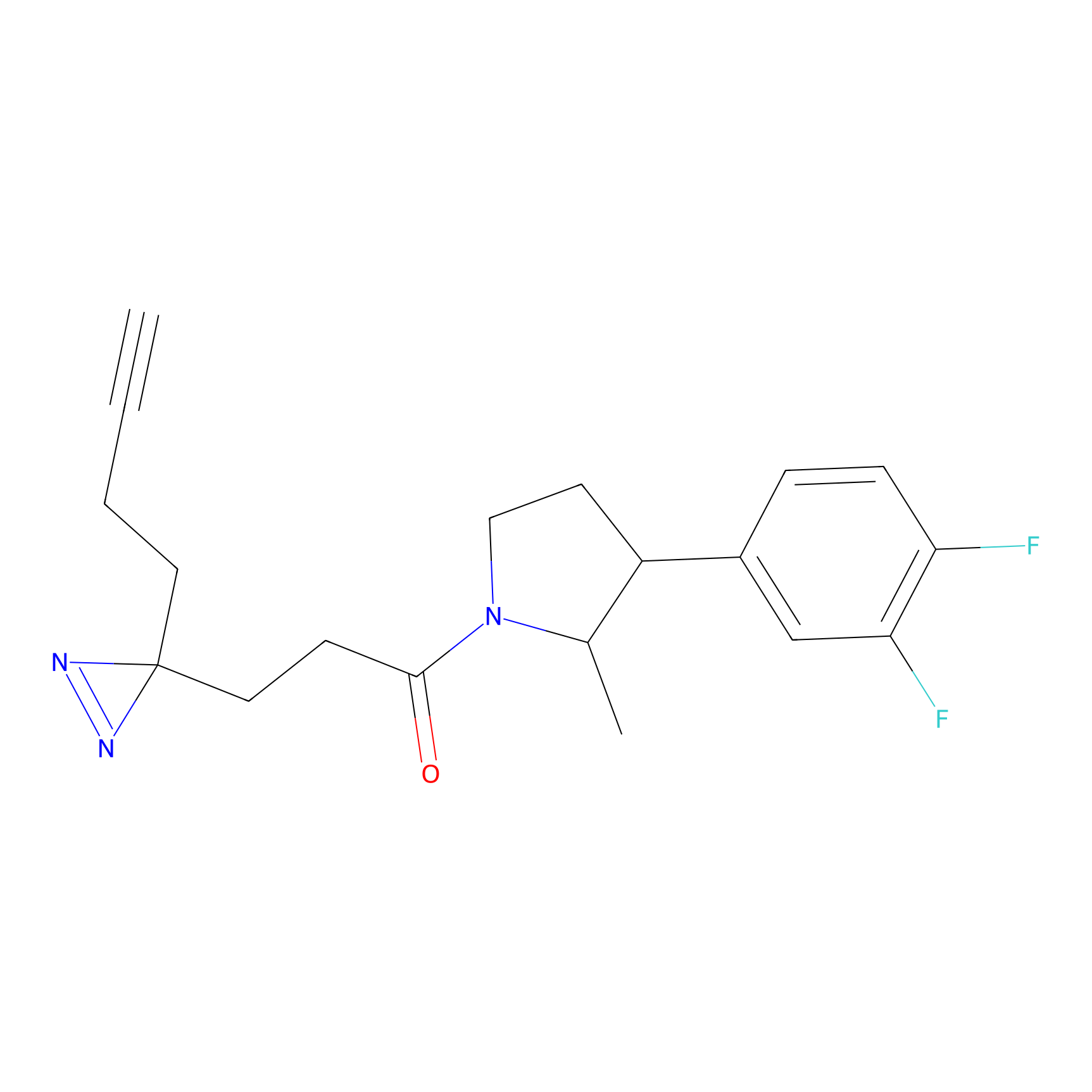
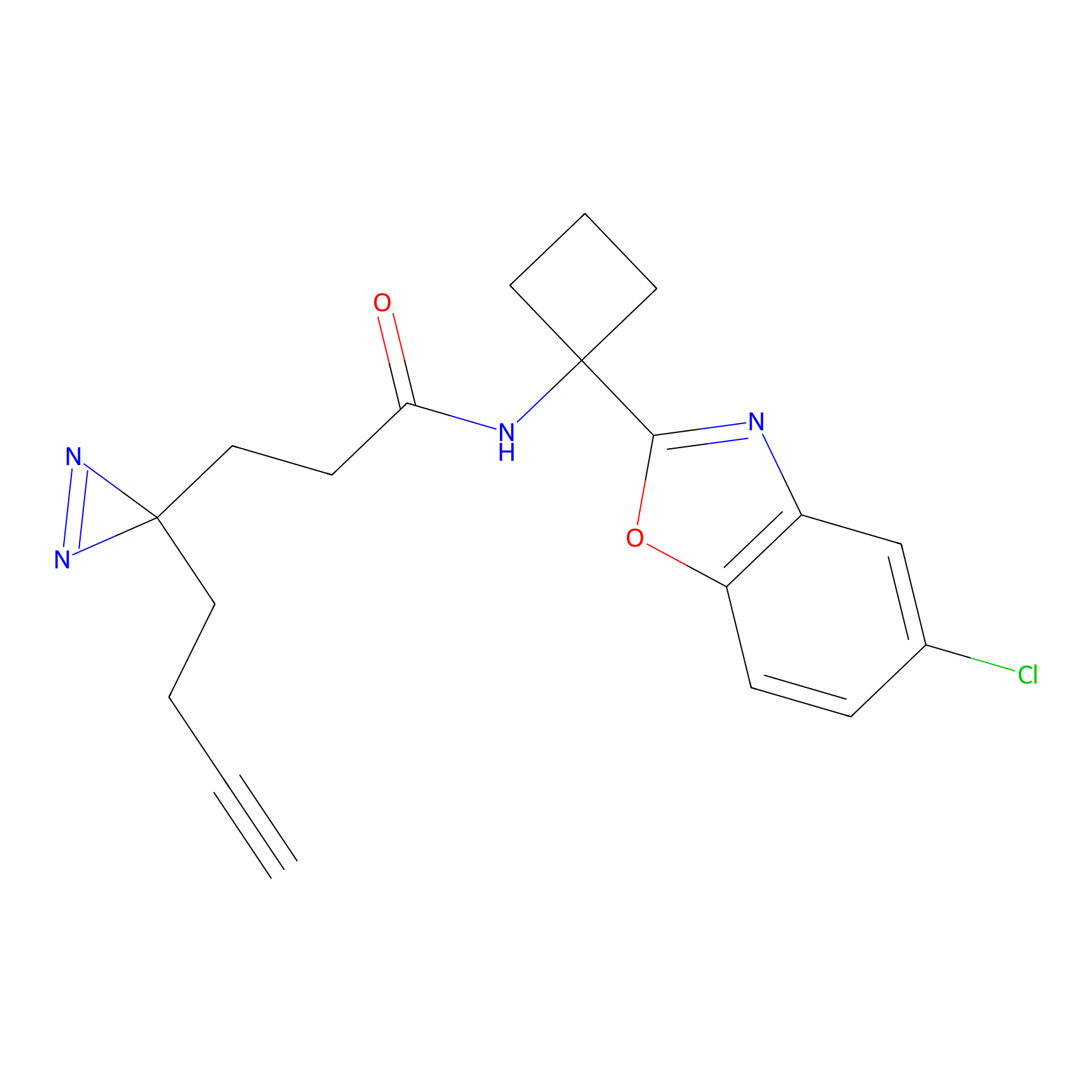
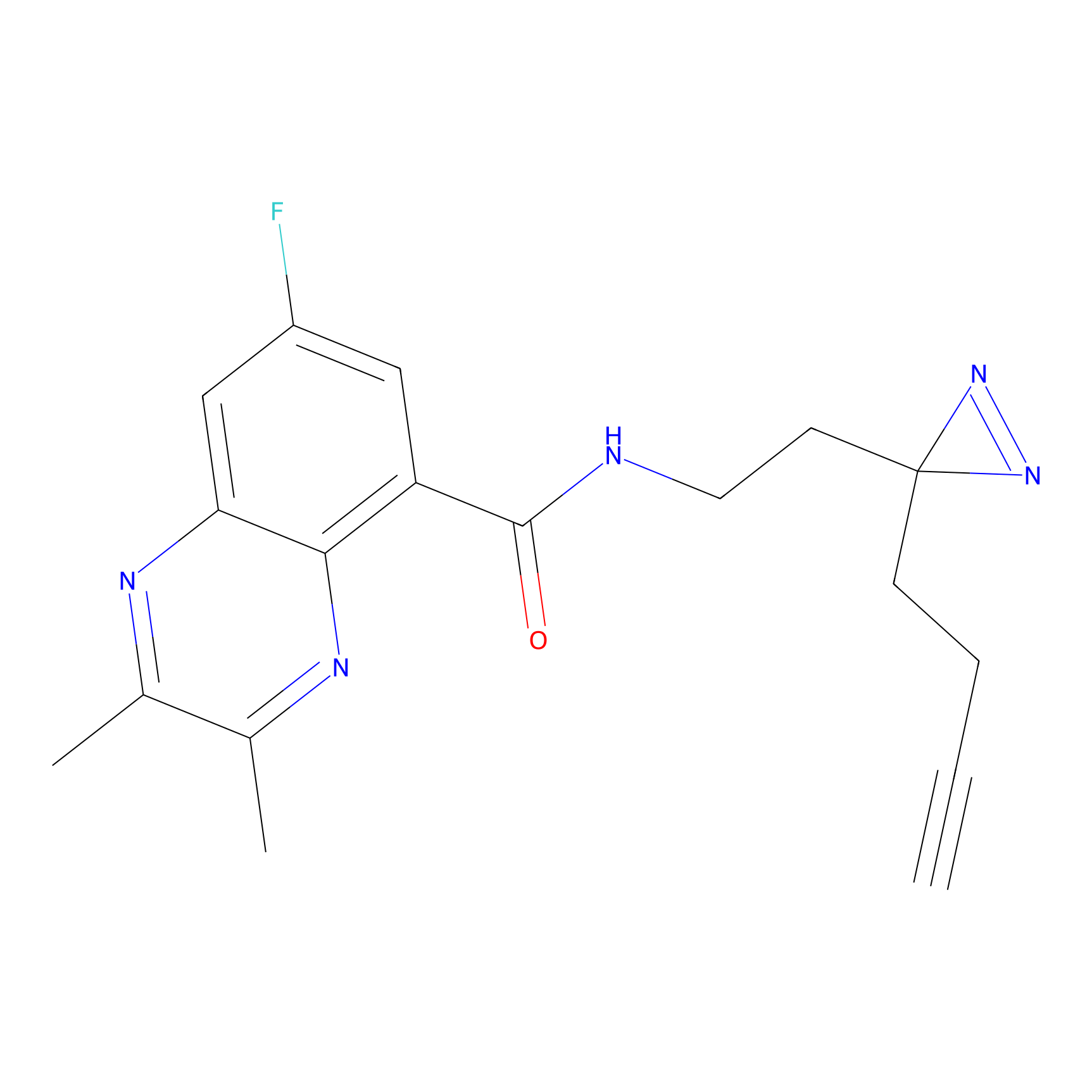
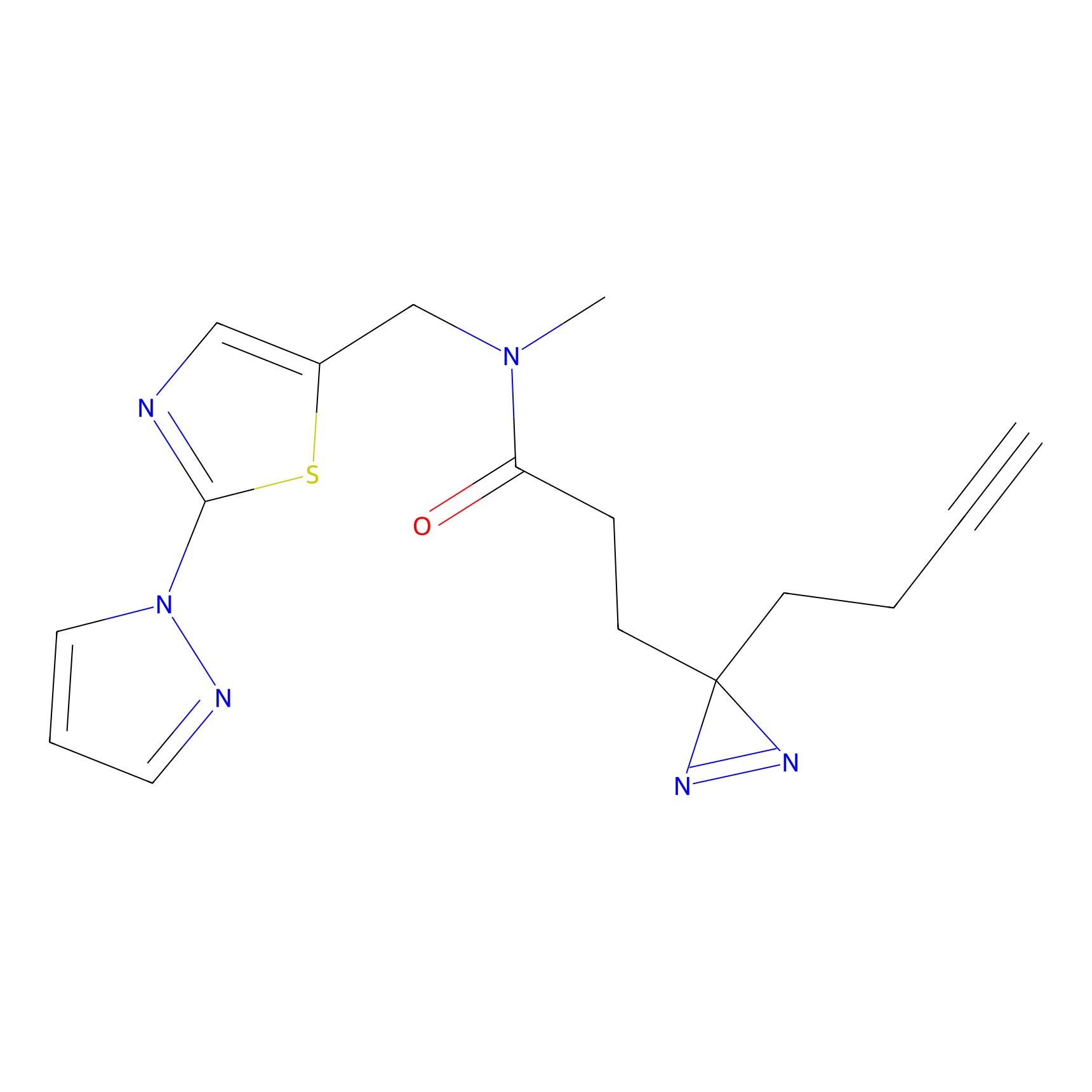
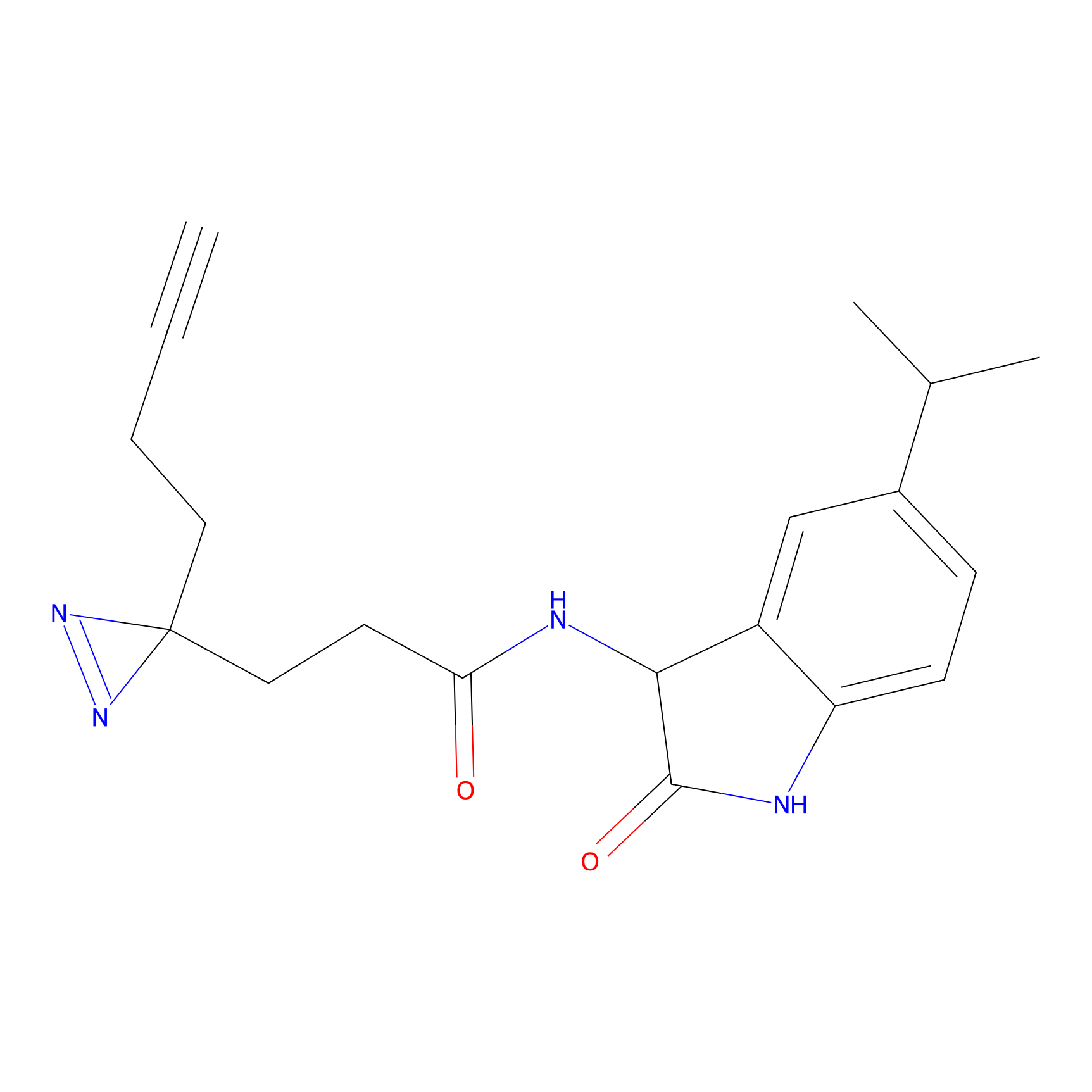
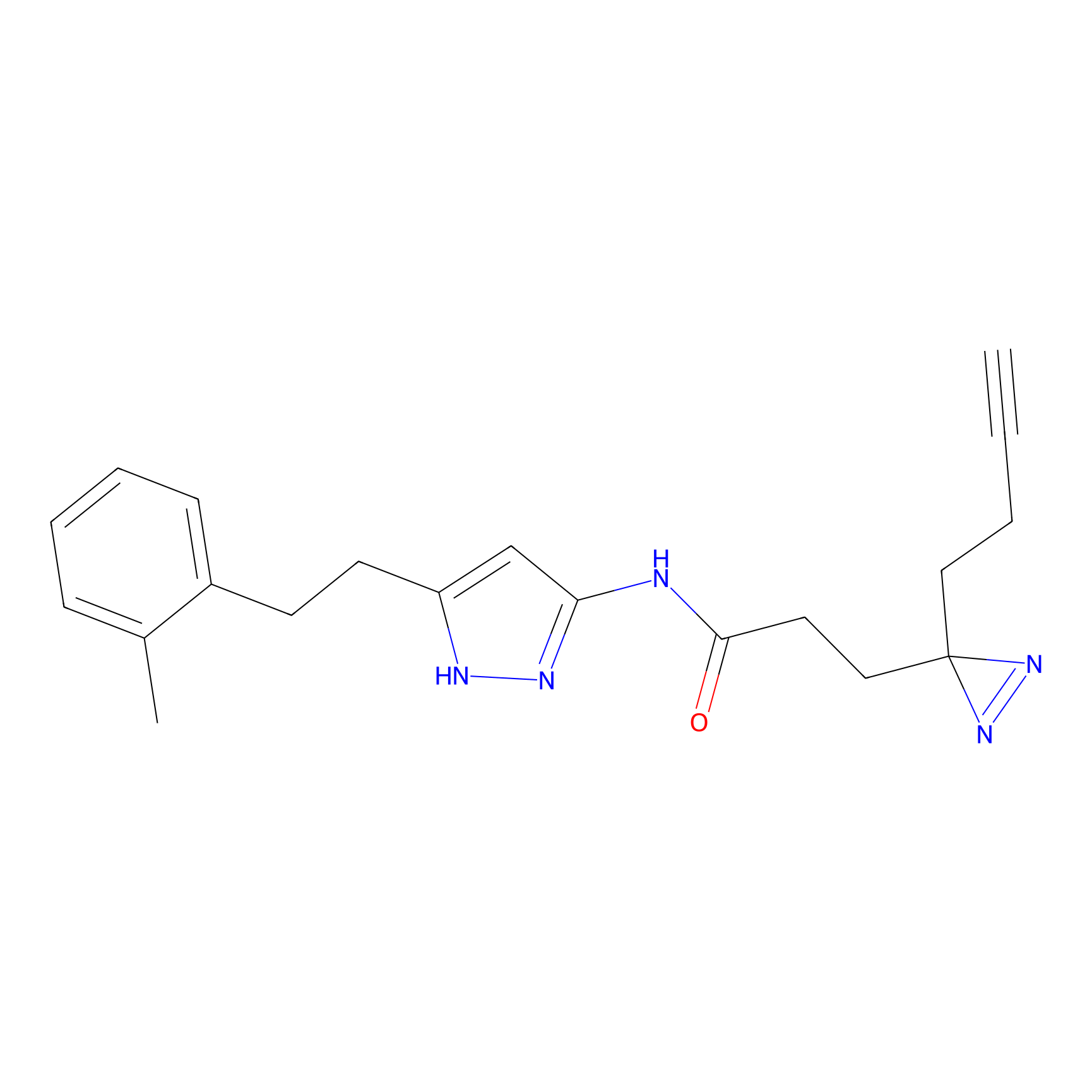
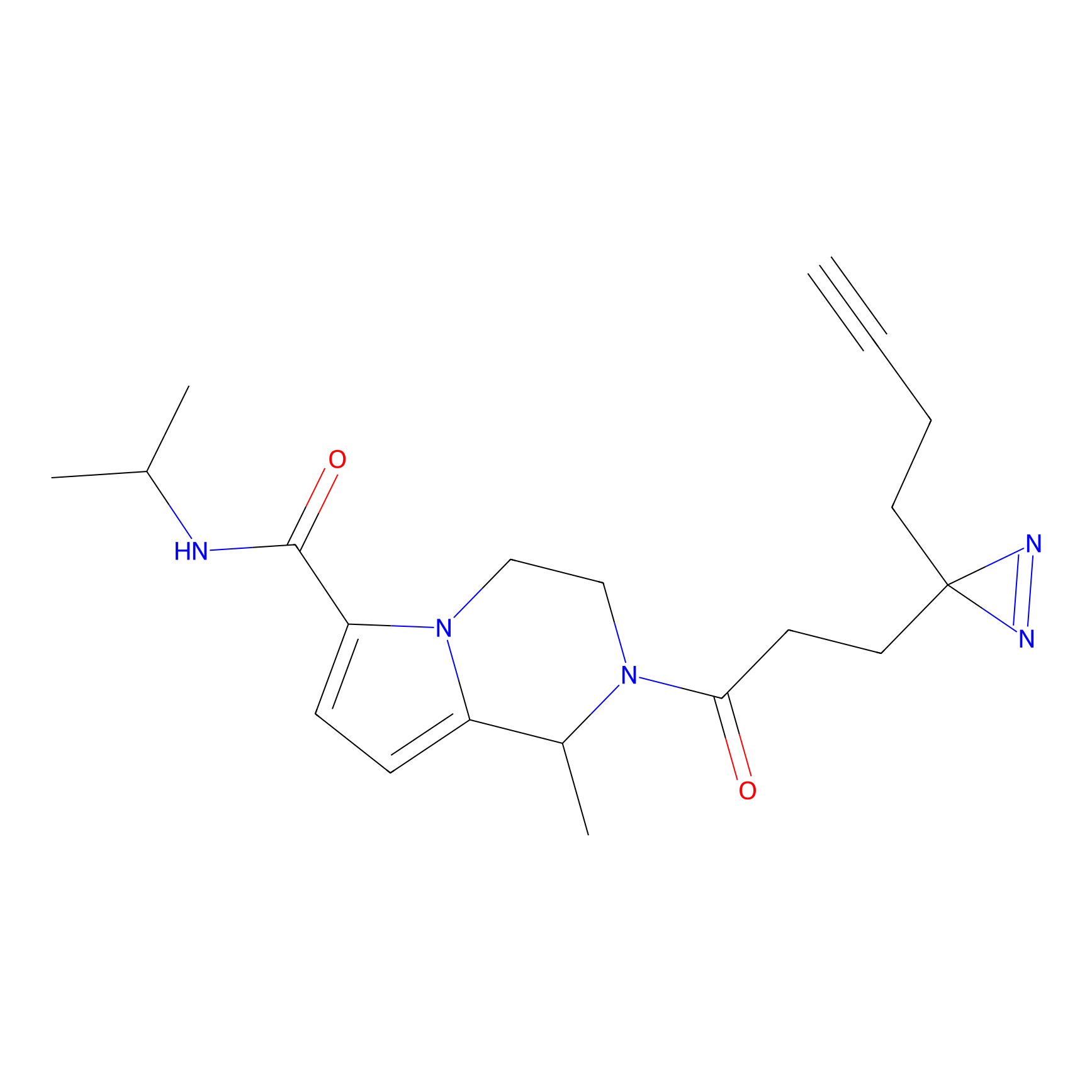
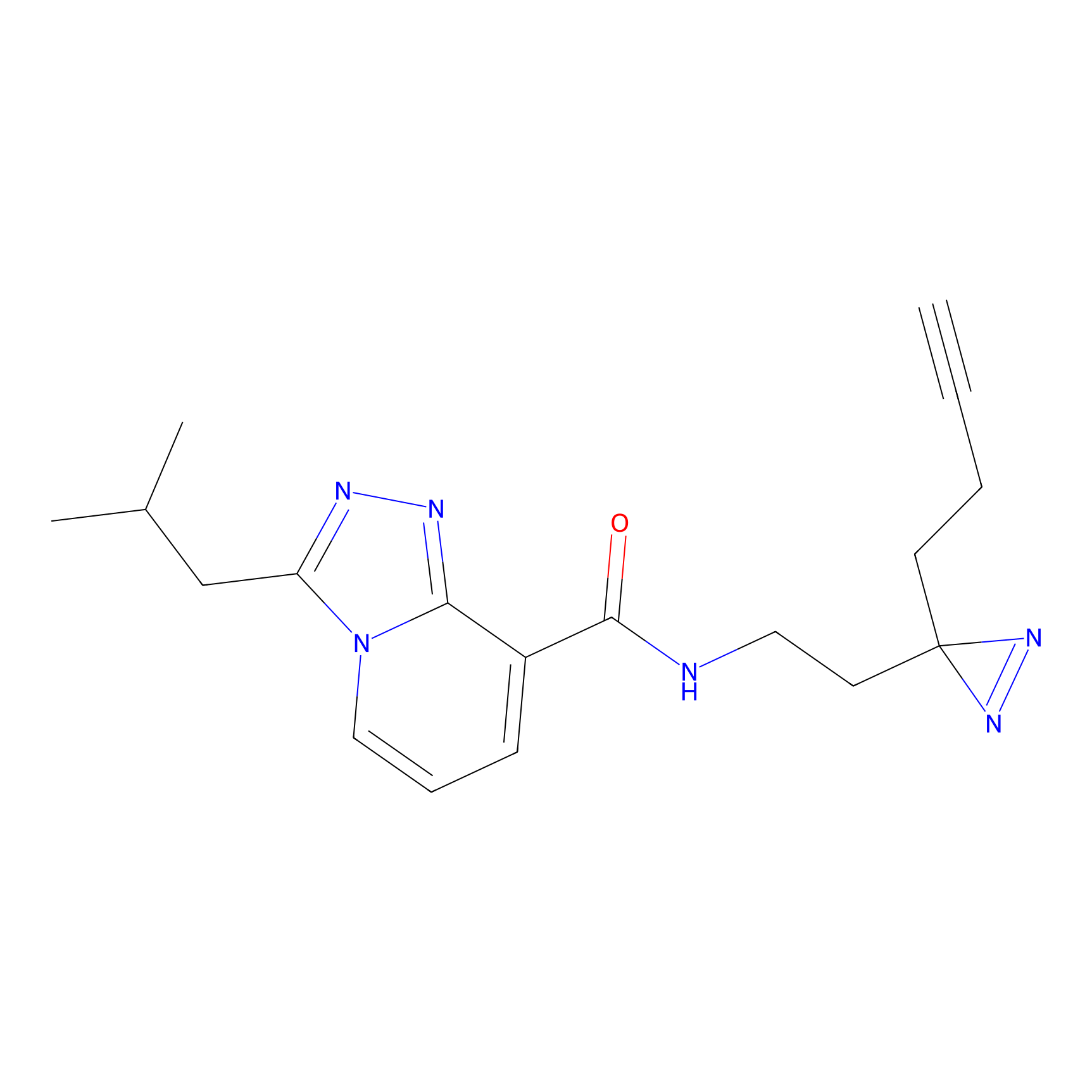
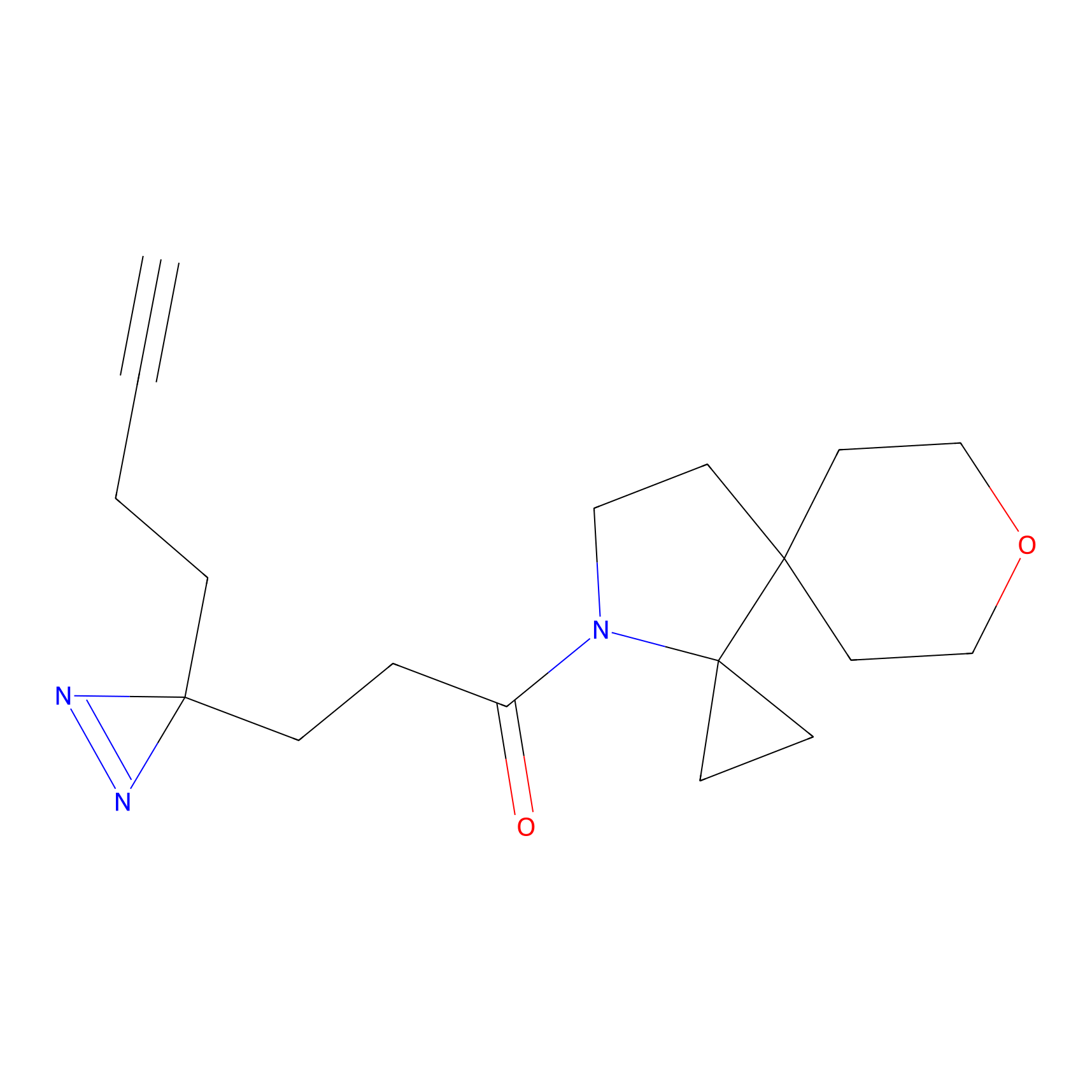
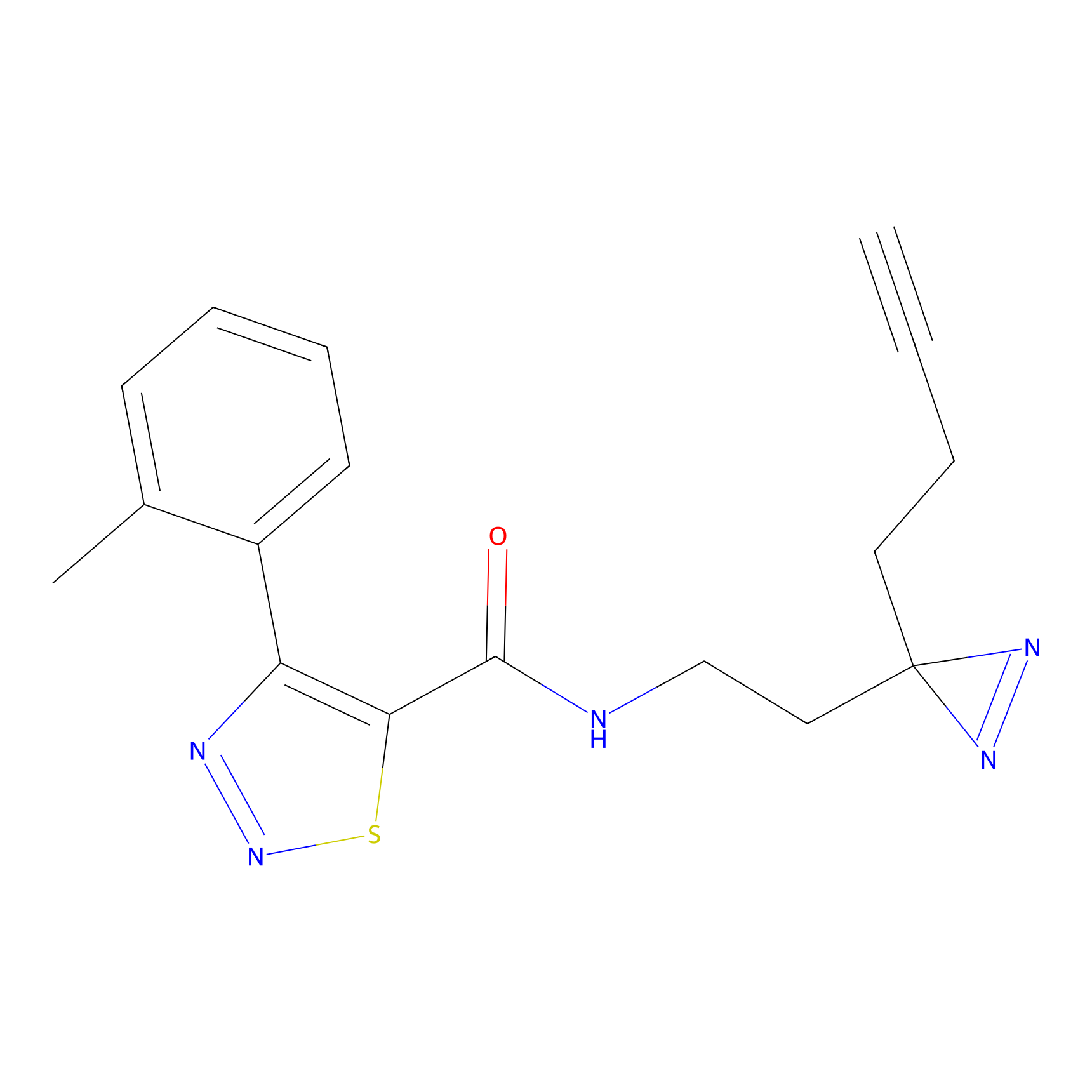
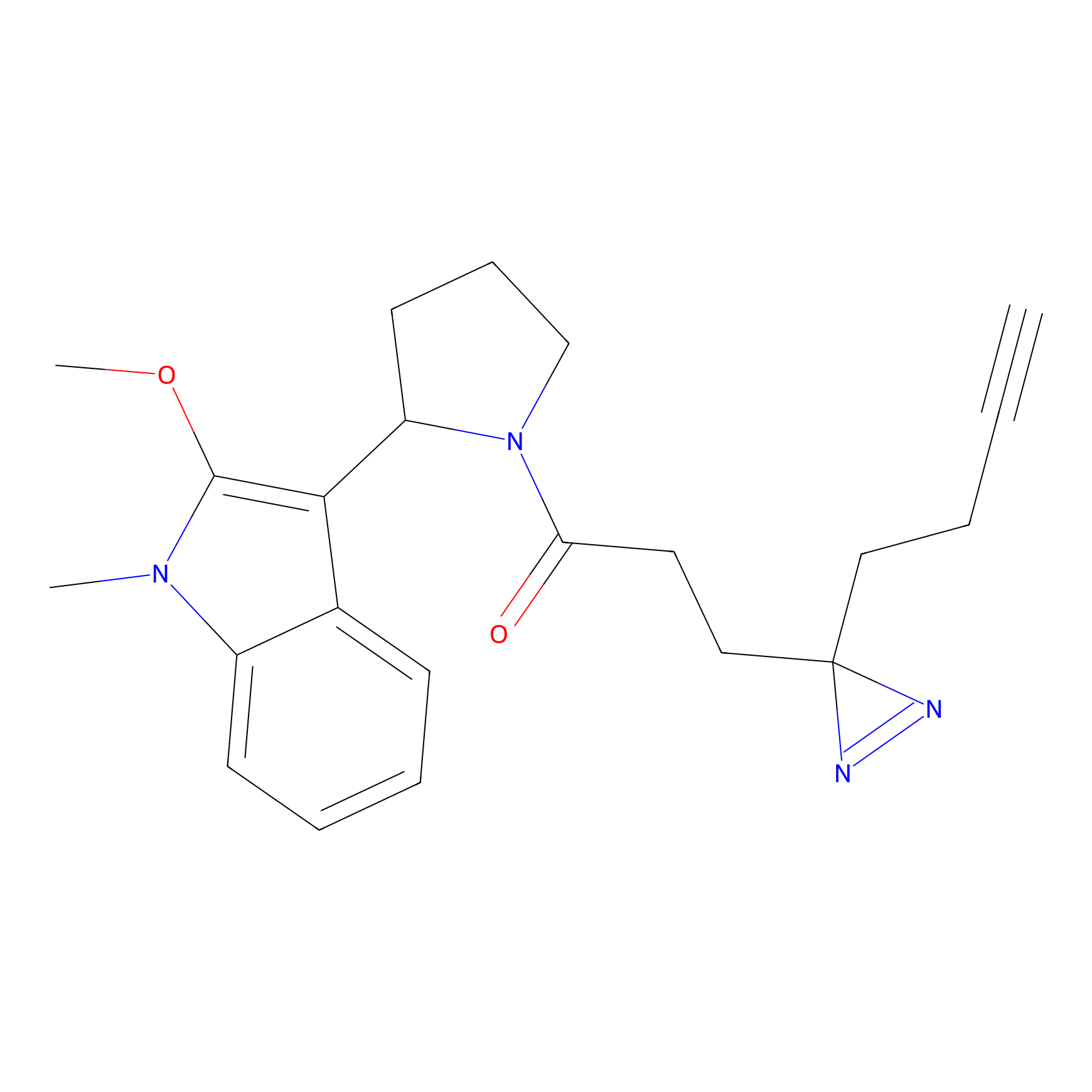
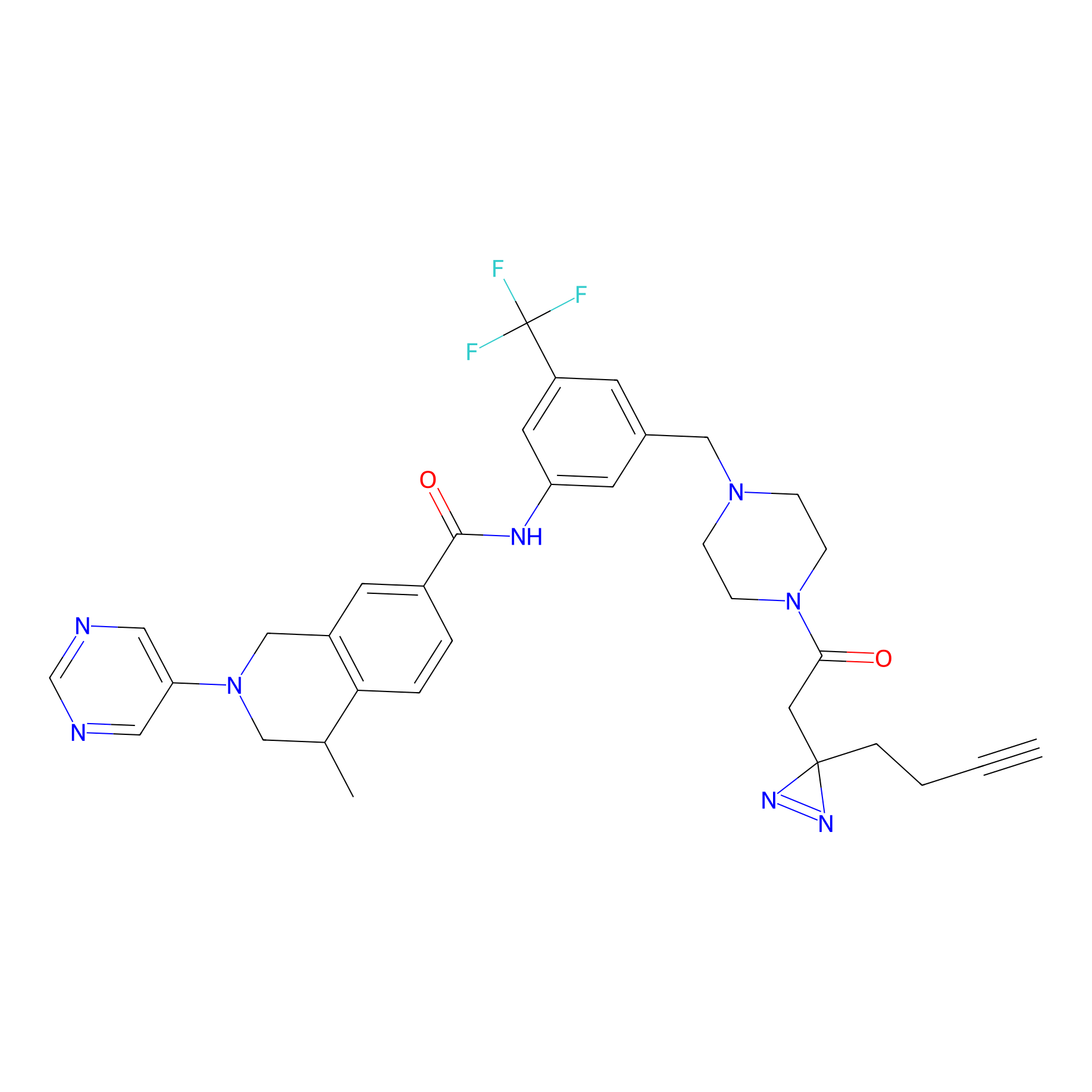
DBIA Probe Info |
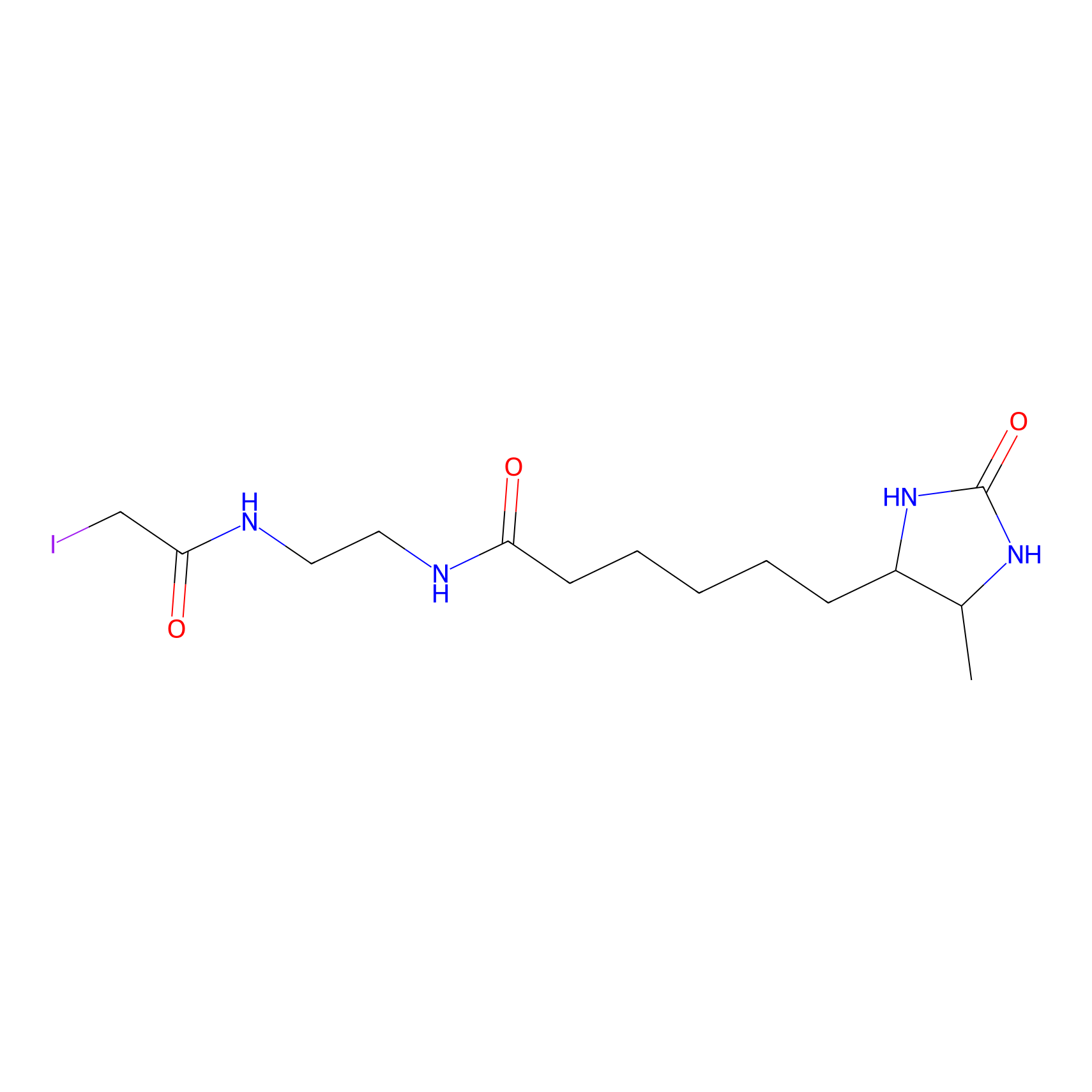 |
C109(1.35) | LDD1576 | [4] | |
|
Acrolein Probe Info |
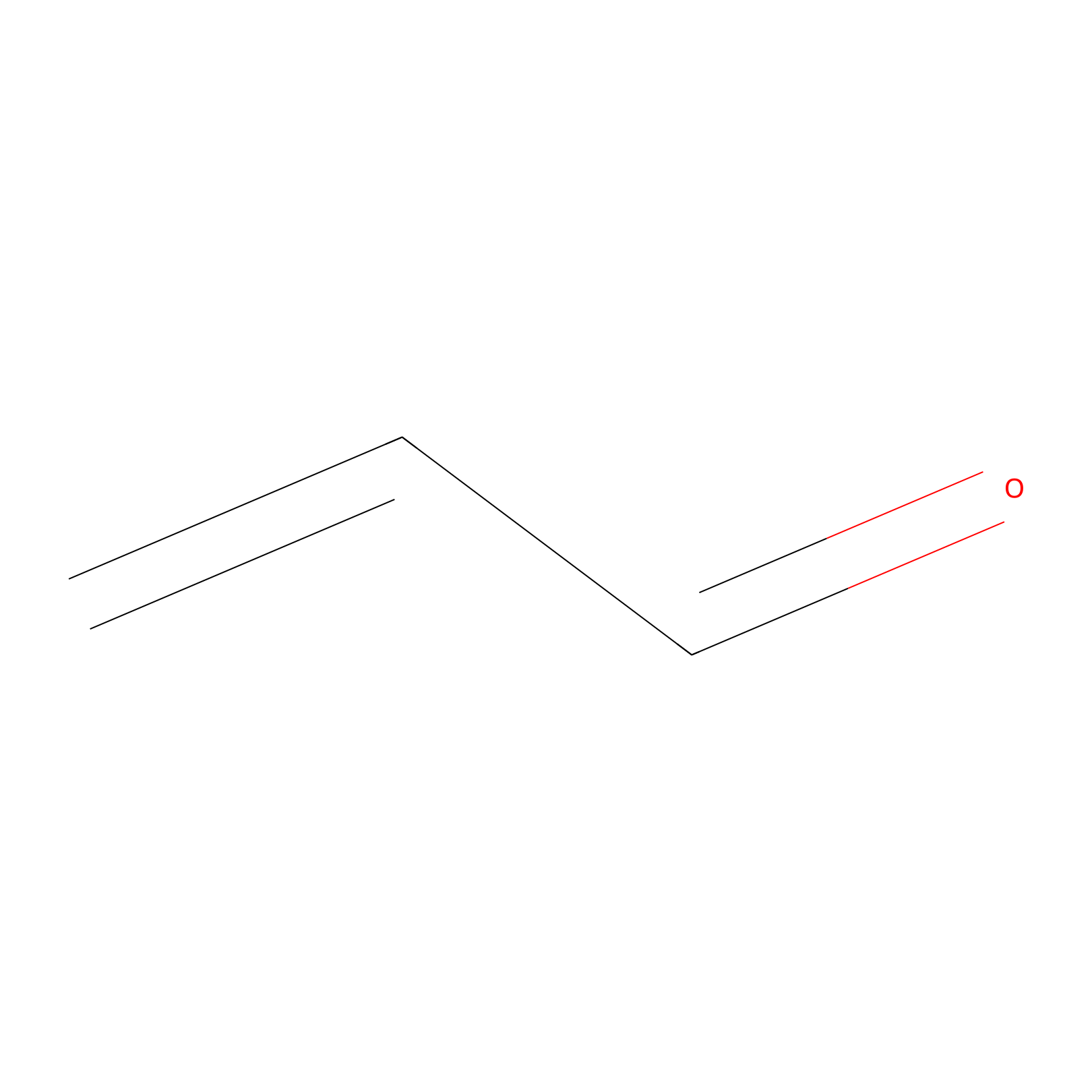 |
N.A. | LDD0217 | [5] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0083 | Avasimibe | A-549 | 2.62 | LDD0143 | [9] |
| LDCM0108 | Chloroacetamide | HeLa | H425(0.00); H360(0.00); K365(0.00) | LDD0222 | [5] |
| LDCM0372 | CL103 | HEK-293T | C109(1.35) | LDD1576 | [4] |
| LDCM0376 | CL107 | HEK-293T | C109(1.19) | LDD1580 | [4] |
| LDCM0381 | CL111 | HEK-293T | C109(1.30) | LDD1585 | [4] |
| LDCM0385 | CL115 | HEK-293T | C109(1.32) | LDD1589 | [4] |
| LDCM0389 | CL119 | HEK-293T | C109(1.21) | LDD1593 | [4] |
| LDCM0394 | CL123 | HEK-293T | C109(1.33) | LDD1598 | [4] |
| LDCM0398 | CL127 | HEK-293T | C109(1.25) | LDD1602 | [4] |
| LDCM0402 | CL15 | HEK-293T | C109(1.19) | LDD1606 | [4] |
| LDCM0415 | CL27 | HEK-293T | C109(1.42) | LDD1619 | [4] |
| LDCM0418 | CL3 | HEK-293T | C109(1.42) | LDD1622 | [4] |
| LDCM0428 | CL39 | HEK-293T | C109(1.41) | LDD1632 | [4] |
| LDCM0455 | CL63 | HEK-293T | C109(1.49) | LDD1658 | [4] |
| LDCM0481 | CL87 | HEK-293T | C109(1.43) | LDD1684 | [4] |
| LDCM0494 | CL99 | HEK-293T | C109(1.33) | LDD1697 | [4] |
| LDCM0152 | DR | NCI-H1299 | 2.01 | LDD0397 | [8] |
| LDCM0495 | E2913 | HEK-293T | C109(1.22) | LDD1698 | [4] |
| LDCM0468 | Fragment33 | HEK-293T | C109(1.53) | LDD1671 | [4] |
| LDCM0107 | IAA | HeLa | H425(0.00); H360(0.00); K365(0.00) | LDD0221 | [5] |
| LDCM0109 | NEM | HeLa | H360(0.00); K365(0.00); H425(0.00) | LDD0223 | [5] |
| LDCM0090 | Rapamycin | JHH-7 | 3.20 | LDD0213 | [10] |
| LDCM0084 | Ro 48-8071 | A-549 | 6.46 | LDD0145 | [9] |
References