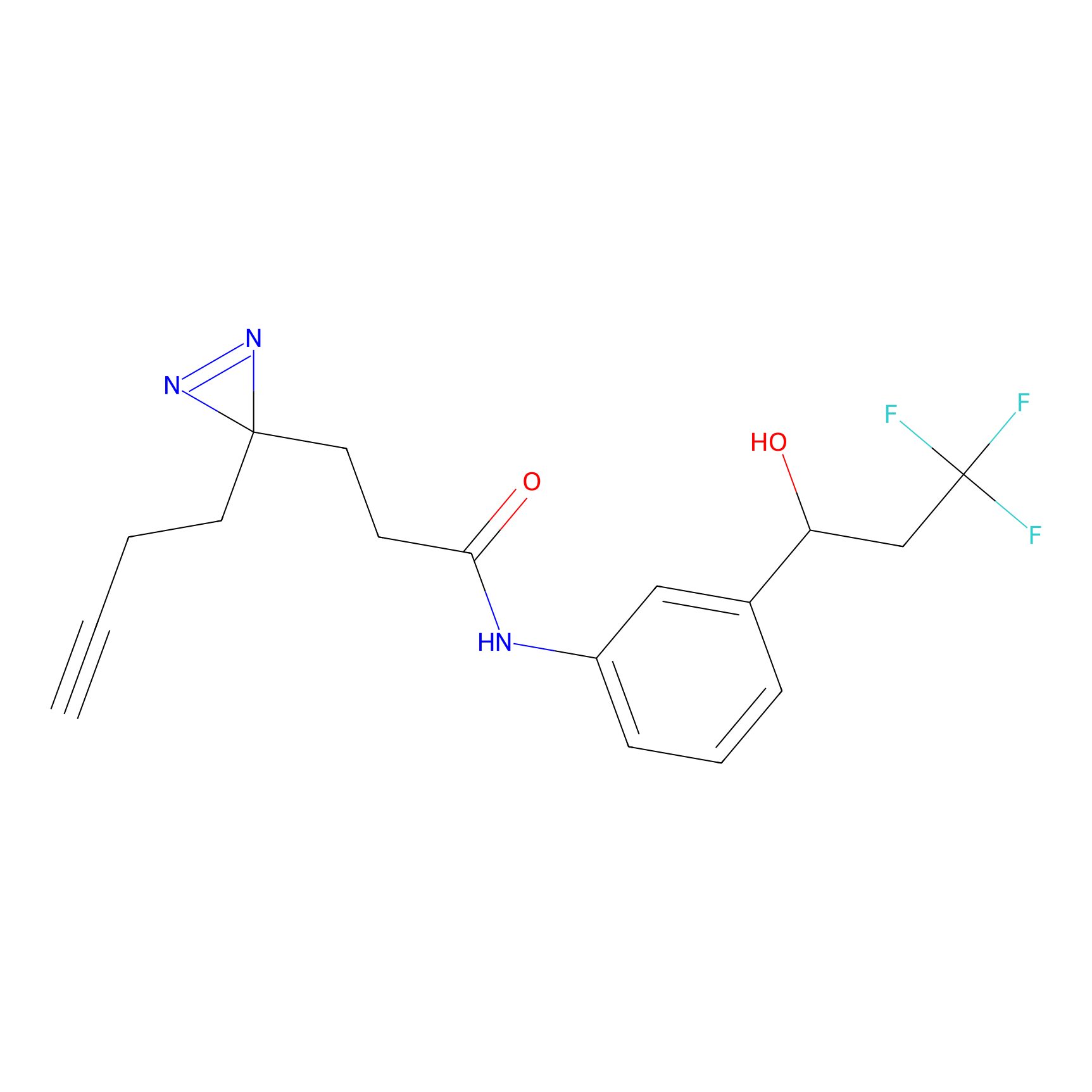
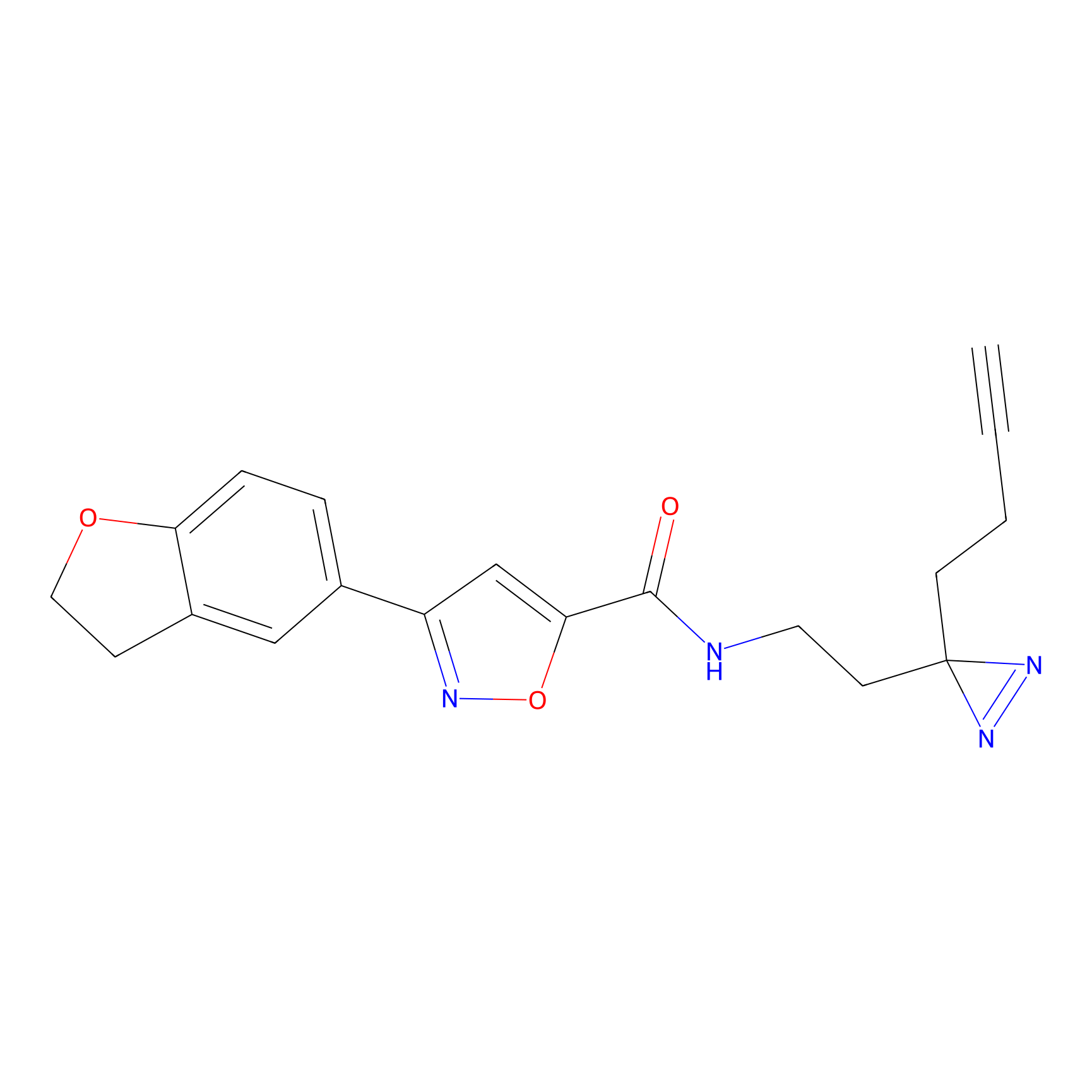
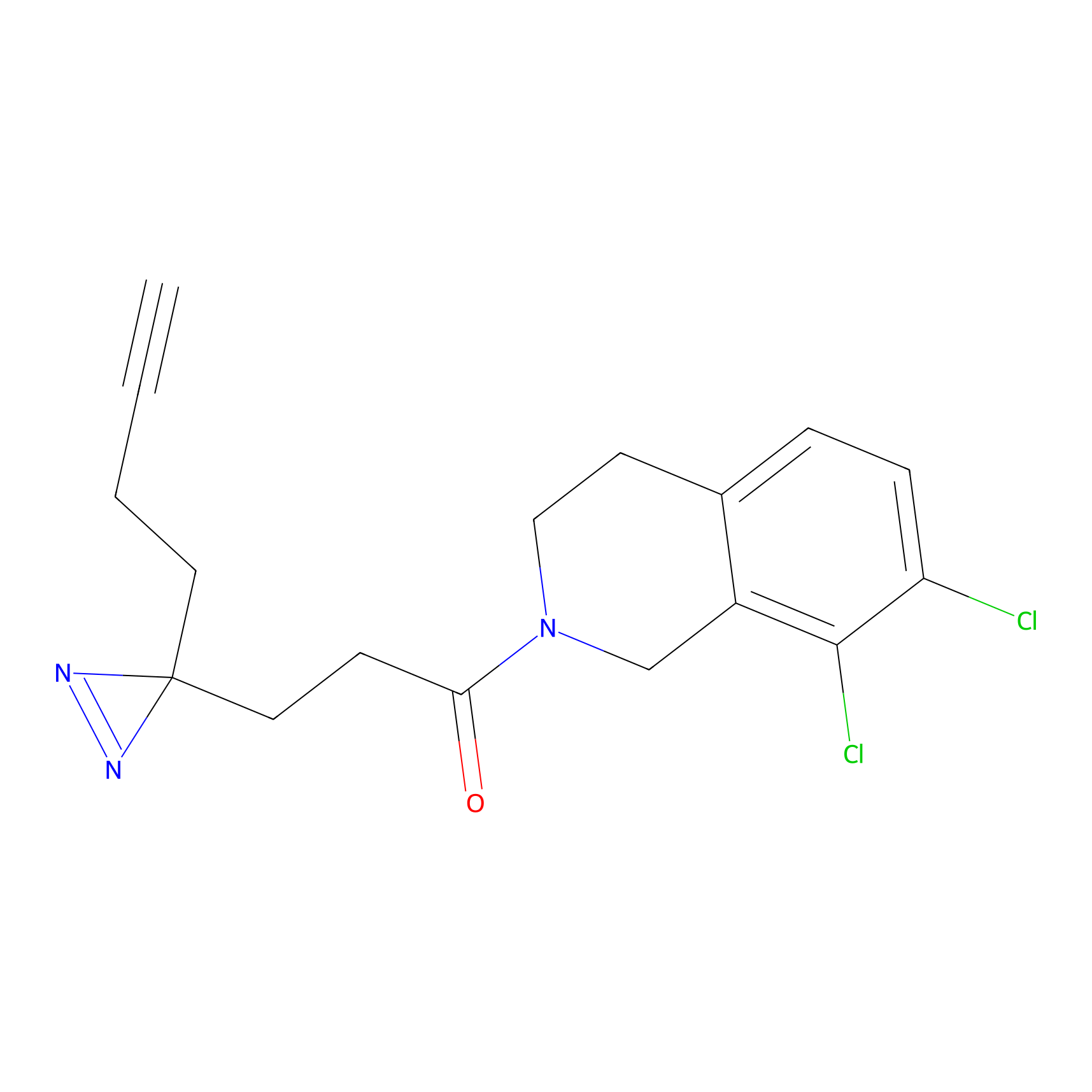
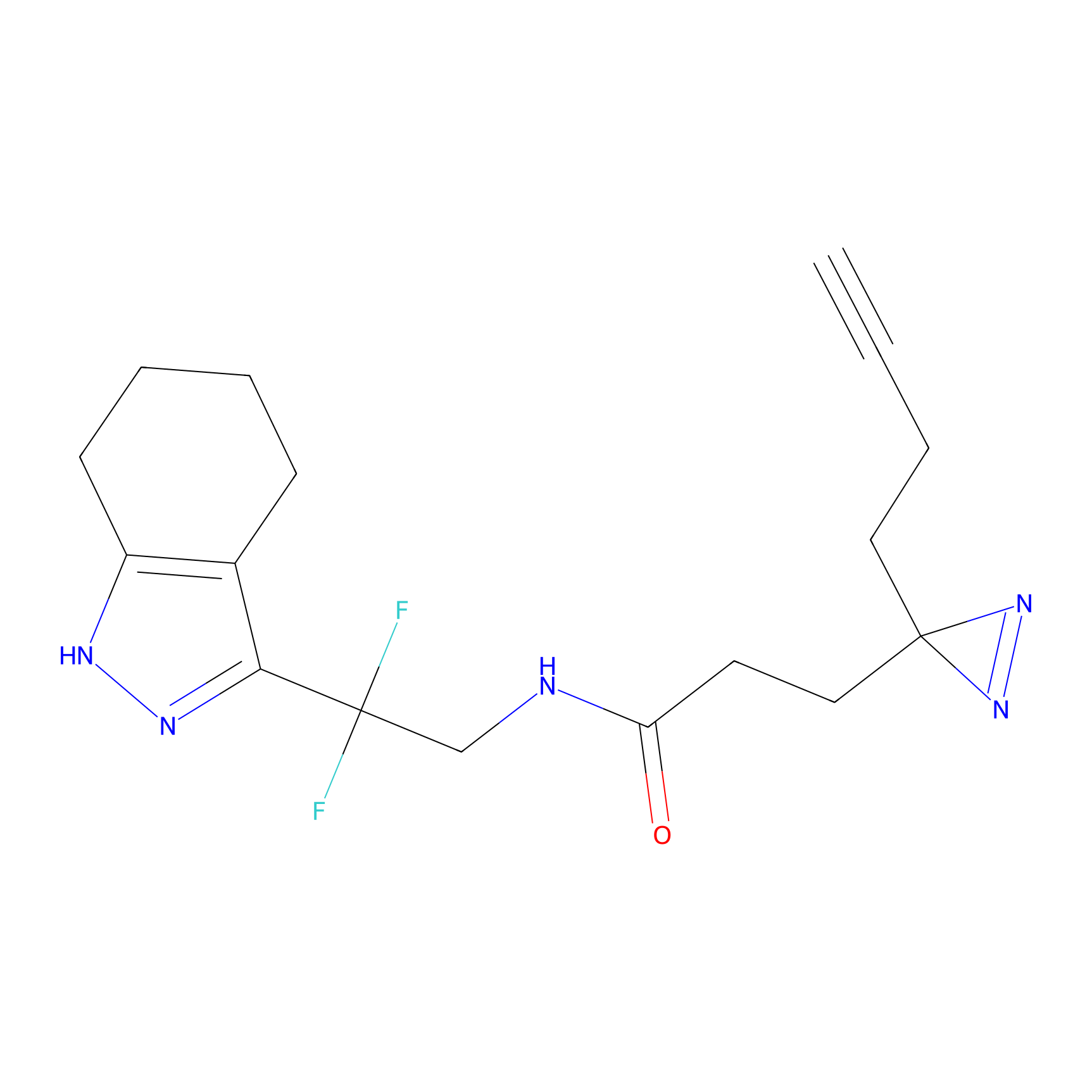
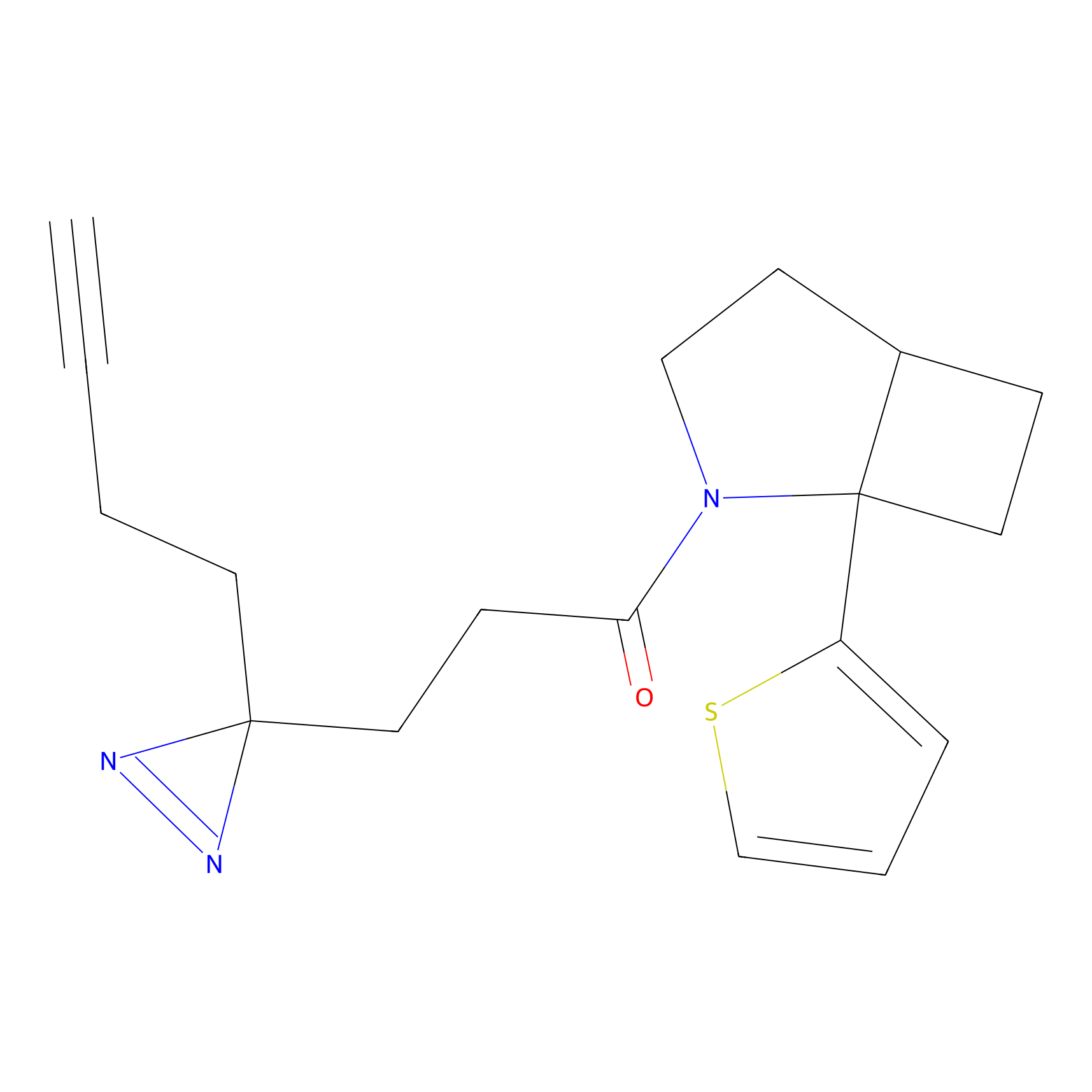
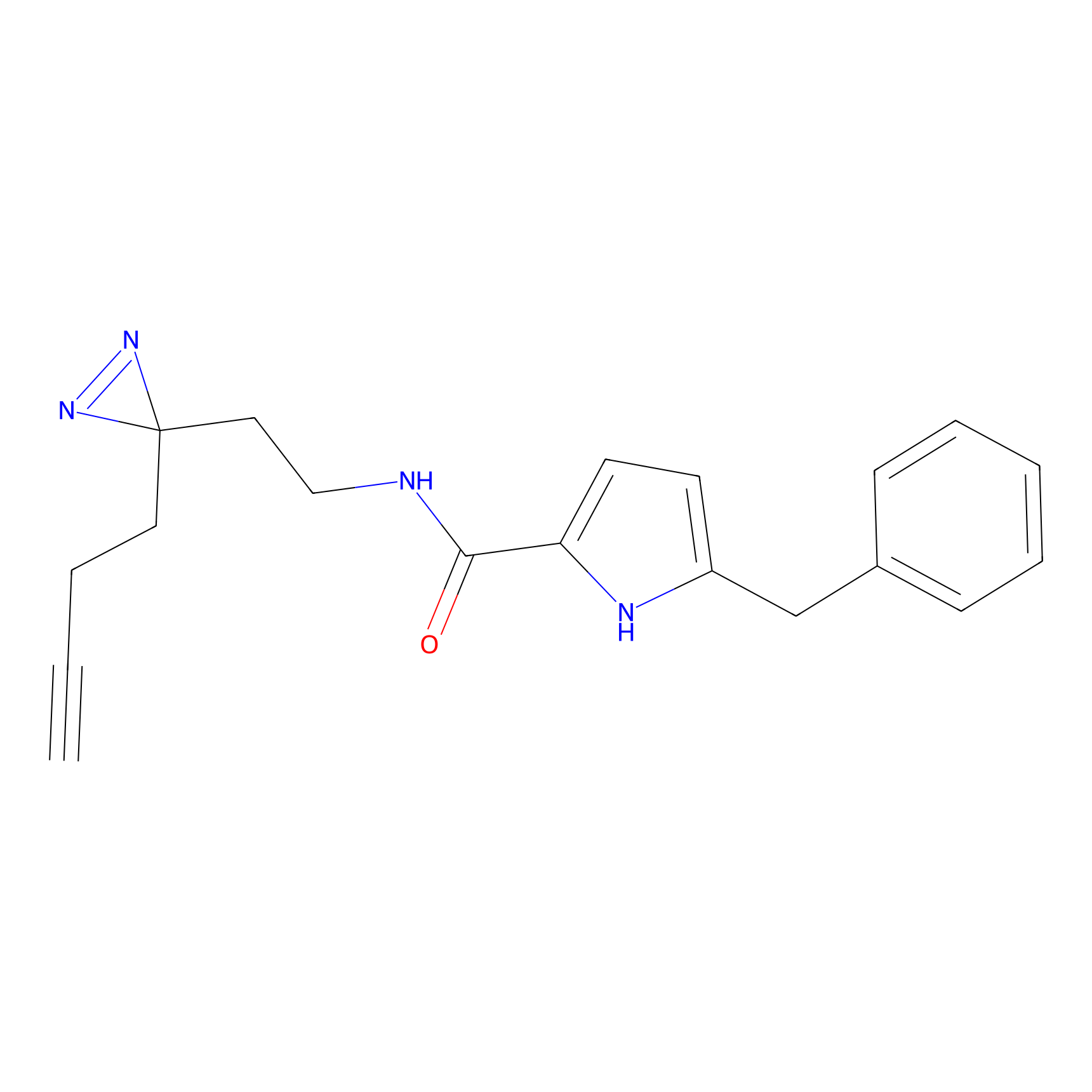
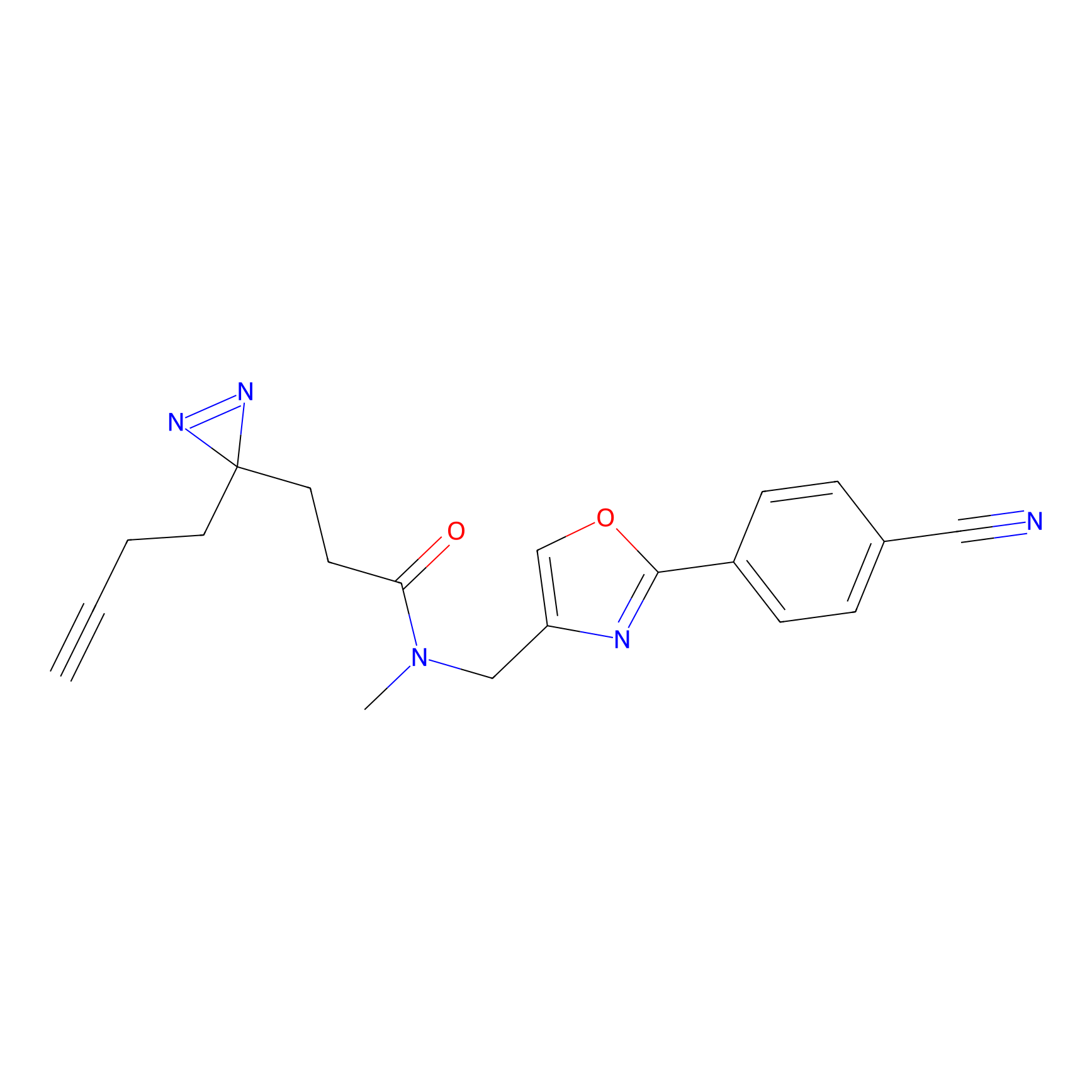
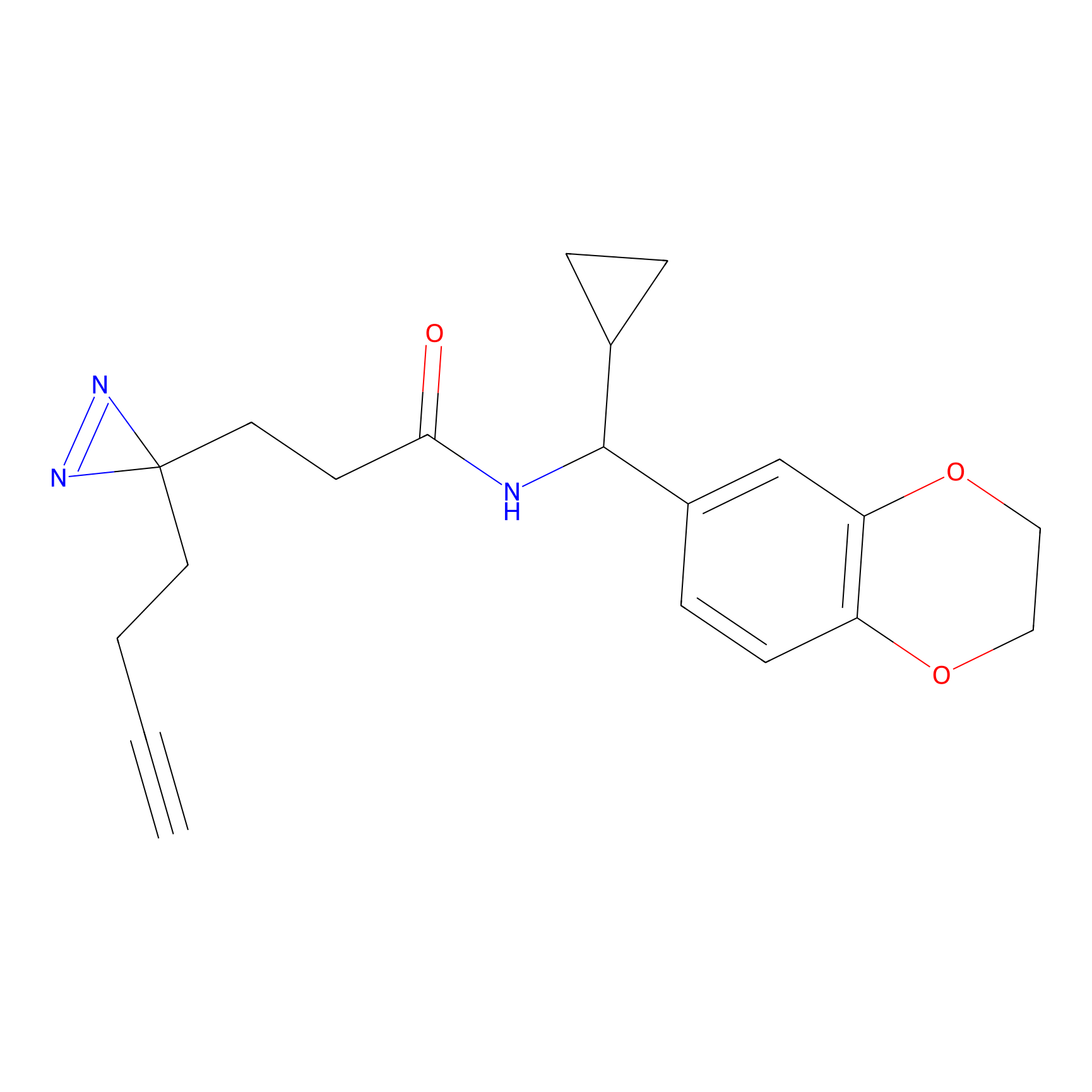
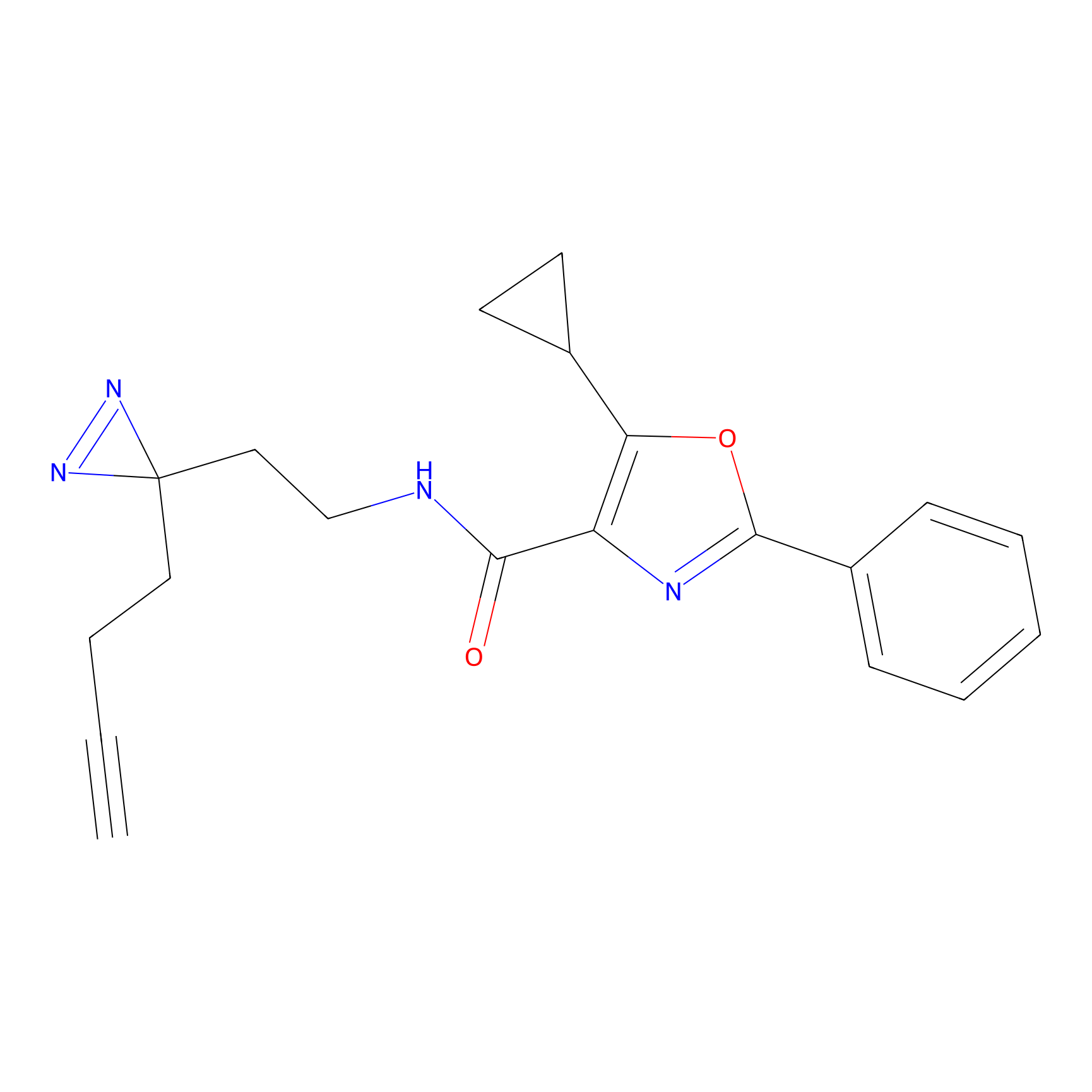
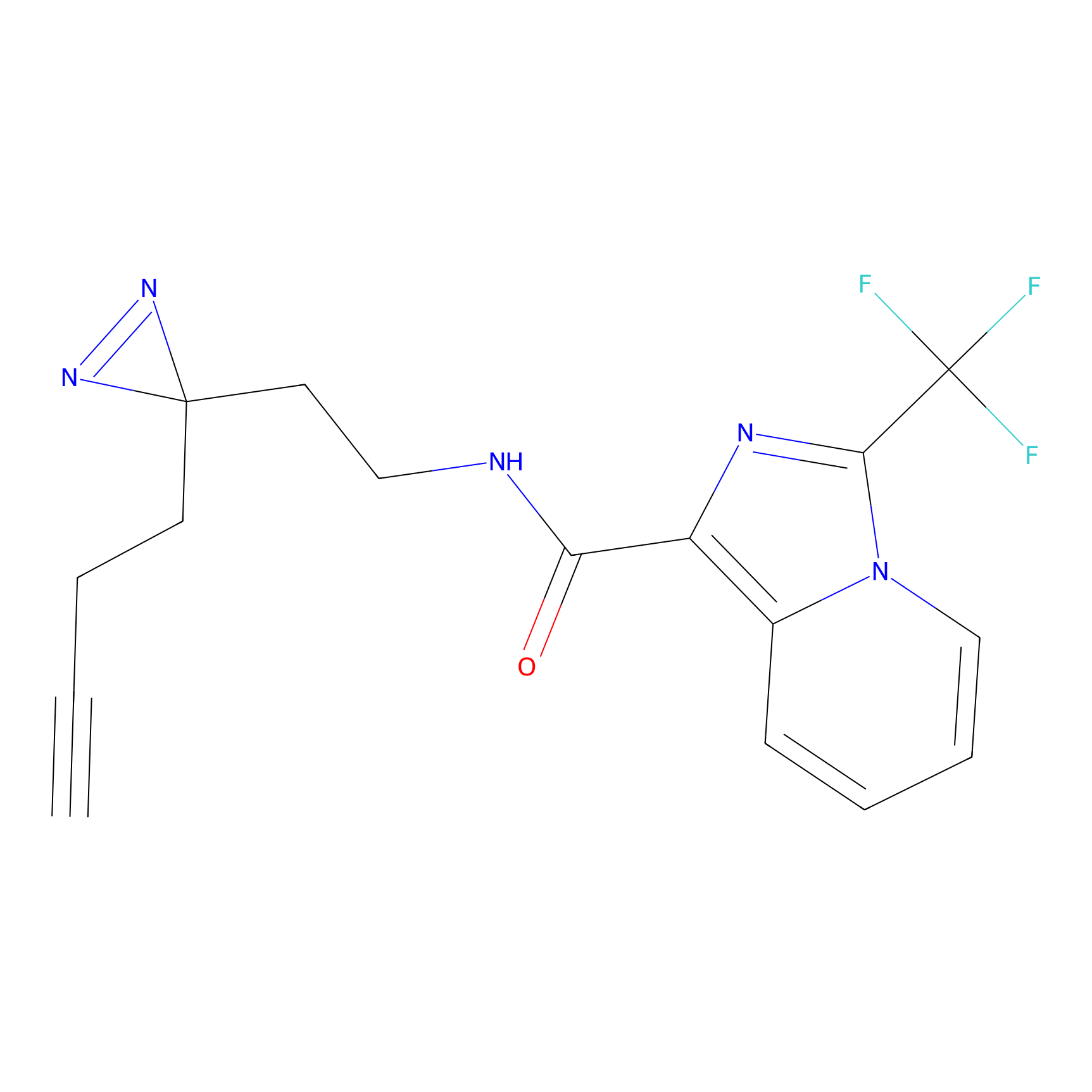
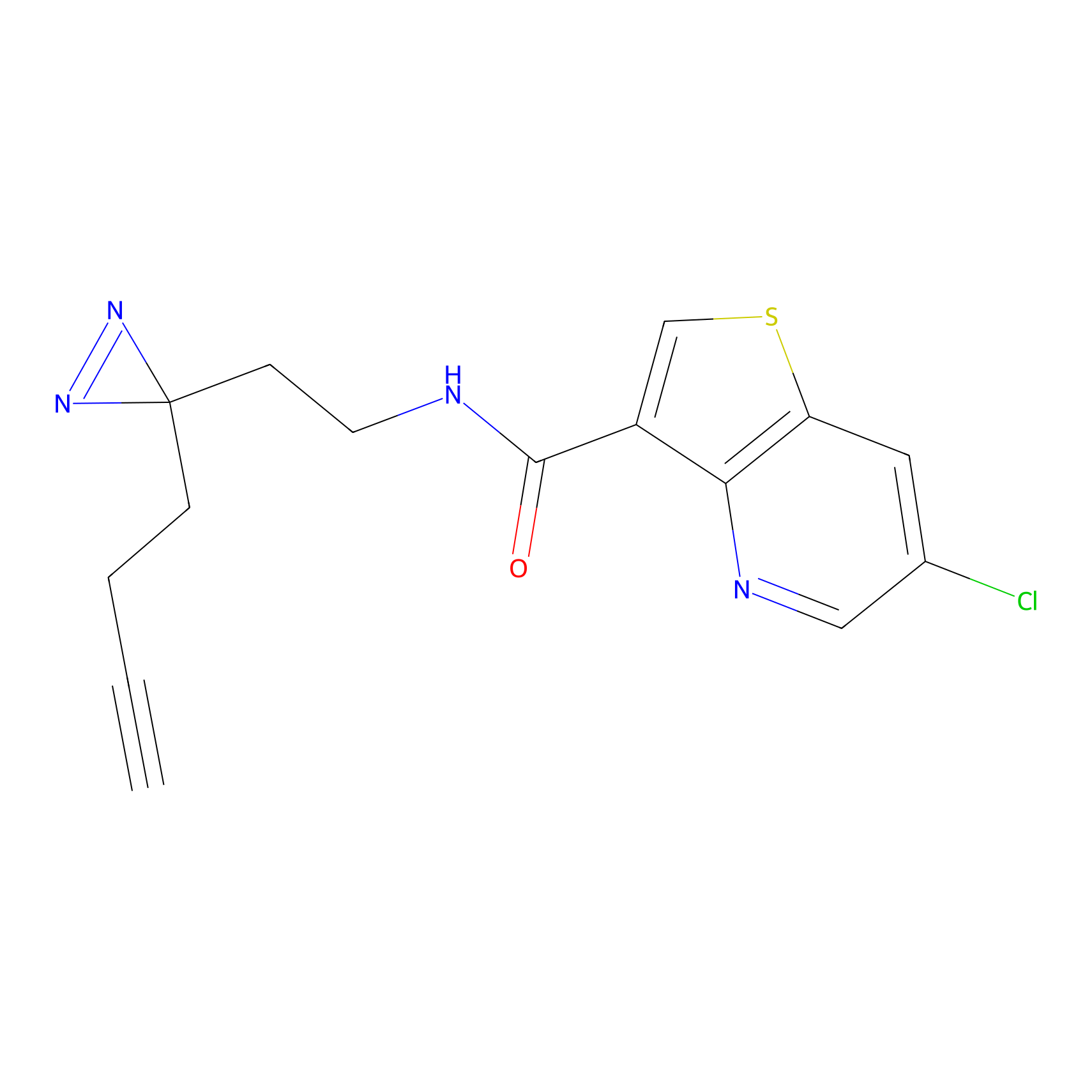
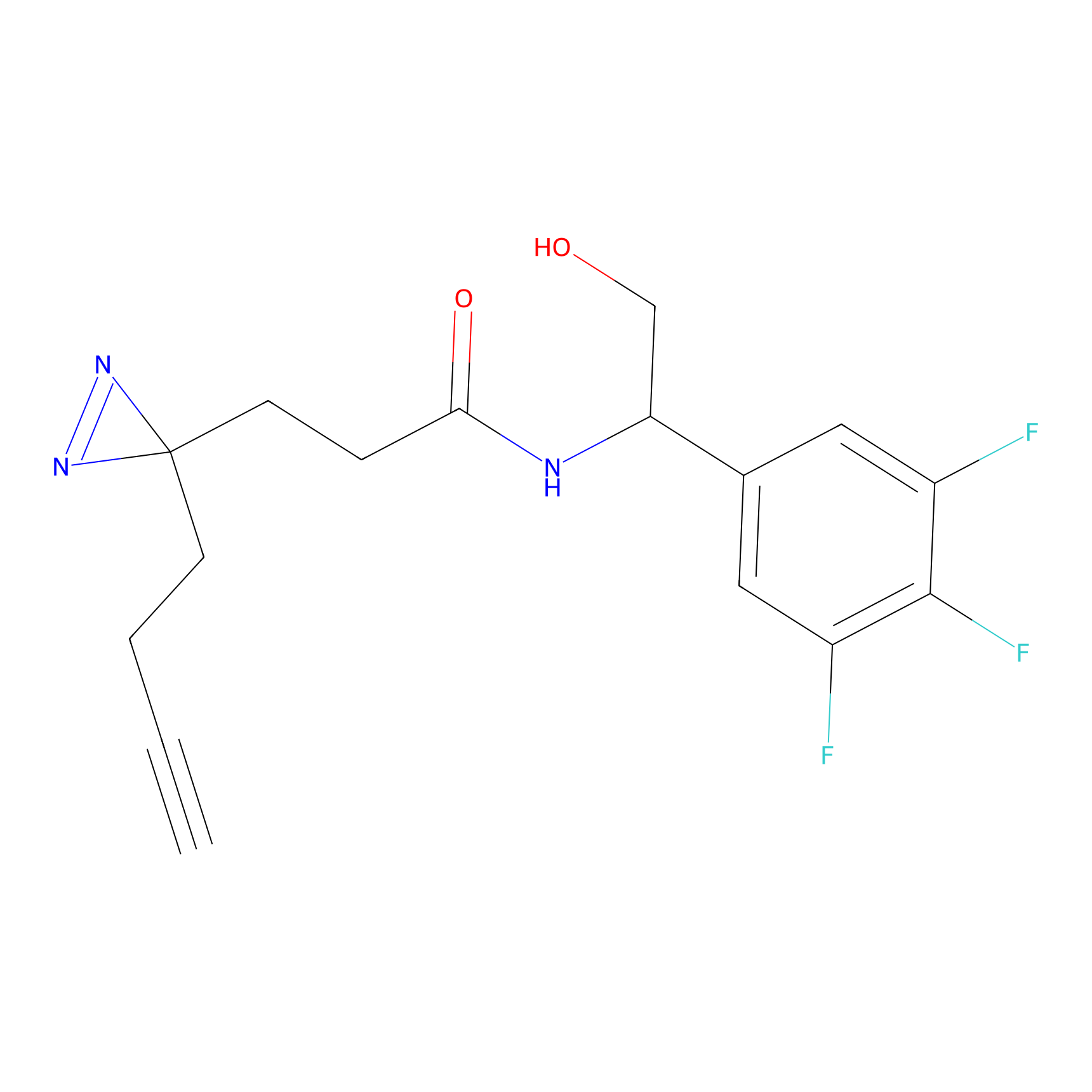
Details of the Target
General Information of Target
| Target ID | LDTP15067 | |||||
|---|---|---|---|---|---|---|
| Target Name | Ubiquinol-cytochrome c reductase complex assembly factor 6 (UQCC6) | |||||
| Gene Name | UQCC6 | |||||
| Gene ID | 728568 | |||||
| Synonyms |
BR; BRAWNIN; C12orf73; Ubiquinol-cytochrome c reductase complex assembly factor 6; Protein BRAWNIN |
|||||
| 3D Structure | ||||||
| Sequence |
MAQKPLRLLACGDVEGKFDILFNRVQAIQKKSGNFDLLLCVGNFFGSTQDAEWEEYKTGI
KKAPIQTYVLGANNQETVKYFQDADGCELAENITYLGRKGIFTGSSGLQIVYLSGTESLN EPVPGYSFSPKDVSSLRMMLCTTSQFKGVDILLTSPWPKCVGNFGNSSGEVDTKKCGSAL VSSLATGLKPRYHFAALEKTYYERLPYRNHIILQENAQHATRFIALANVGNPEKKKYLYA FSIVPMKLMDAAELVKQPPDVTENPYRKSGQEASIGKQILAPVEESACQFFFDLNEKQGR KRSSTGRDSKSSPHPKQPRKPPQPPGPCWFCLASPEVEKHLVVNIGTHCYLALAKGGLSD DHVLILPIGHYQSVVELSAEVVEEVEKYKATLRRFFKSRGKWCVVFERNYKSHHLQLQVI PVPISCSTTDDIKDAFITQAQEQQIELLEIPEHSDIKQIAQPGAAYFYVELDTGEKLFHR IKKNFPLQFGREVLASEAILNVPDKSDWRQCQISKEDEETLARRFRKDFEPYDFTLDD |
|||||
| Target Bioclass |
Other
|
|||||
| Family |
UQCC6 family
|
|||||
| Subcellular location |
Mitochondrion inner membrane
|
|||||
| Function |
Required for the assembly and stability of the mitochondrial ubiquinol-cytochrome c reductase complex (complex III (CIII) or cytochrome b-c1 complex), a multisubunit transmembrane complex that is part of the mitochondrial electron transport chain (ETC) which drives oxidative phosphorylation. Mediates early complex III biogenesis. Participates in regulating the levels of electron transport chain proteins, and therefore energy supply, in response to changes in energy demand. Also required for cytochrome c oxidase complex (complex IV) assembly.
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Probe(s) Labeling This Target
ABPP Probe
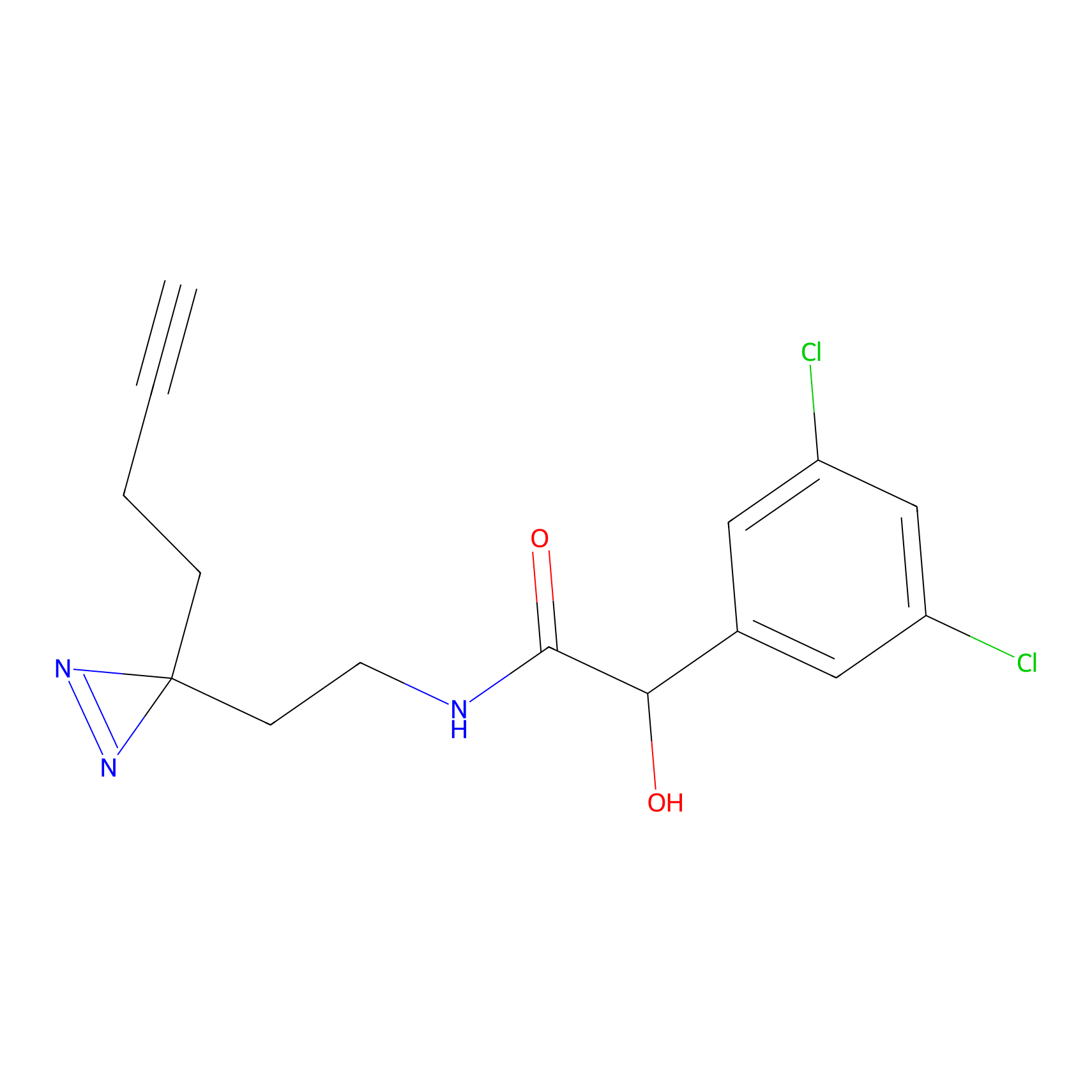
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
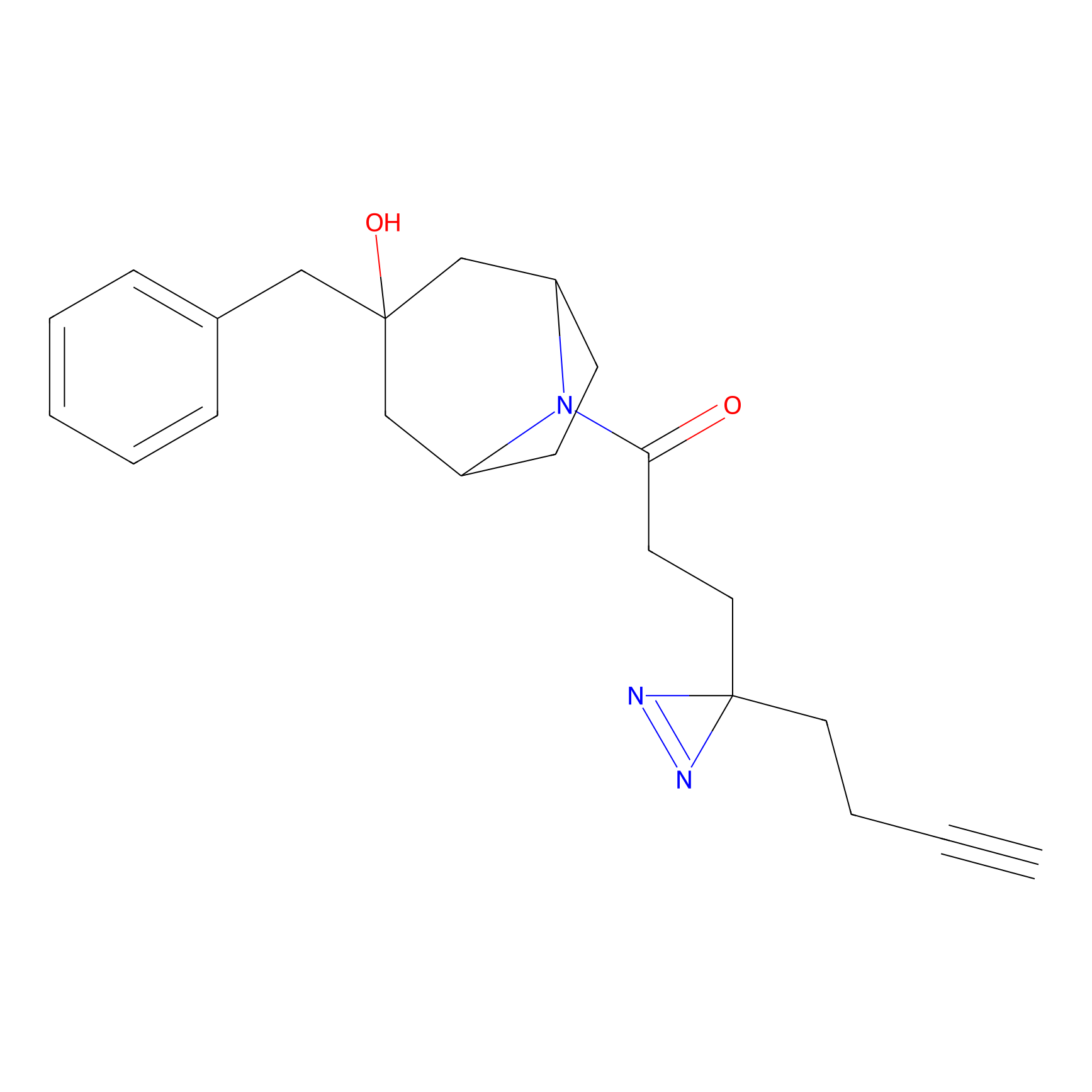
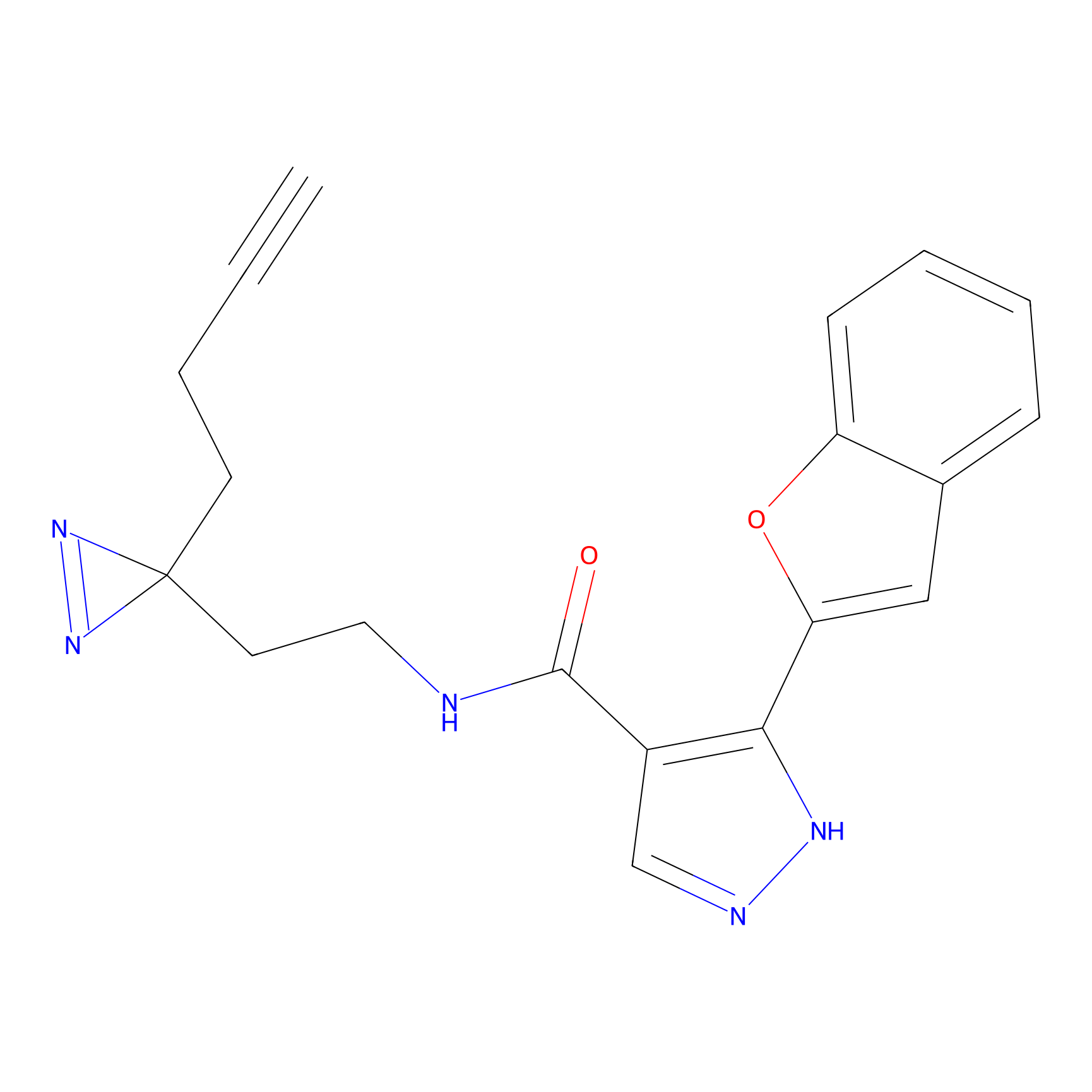
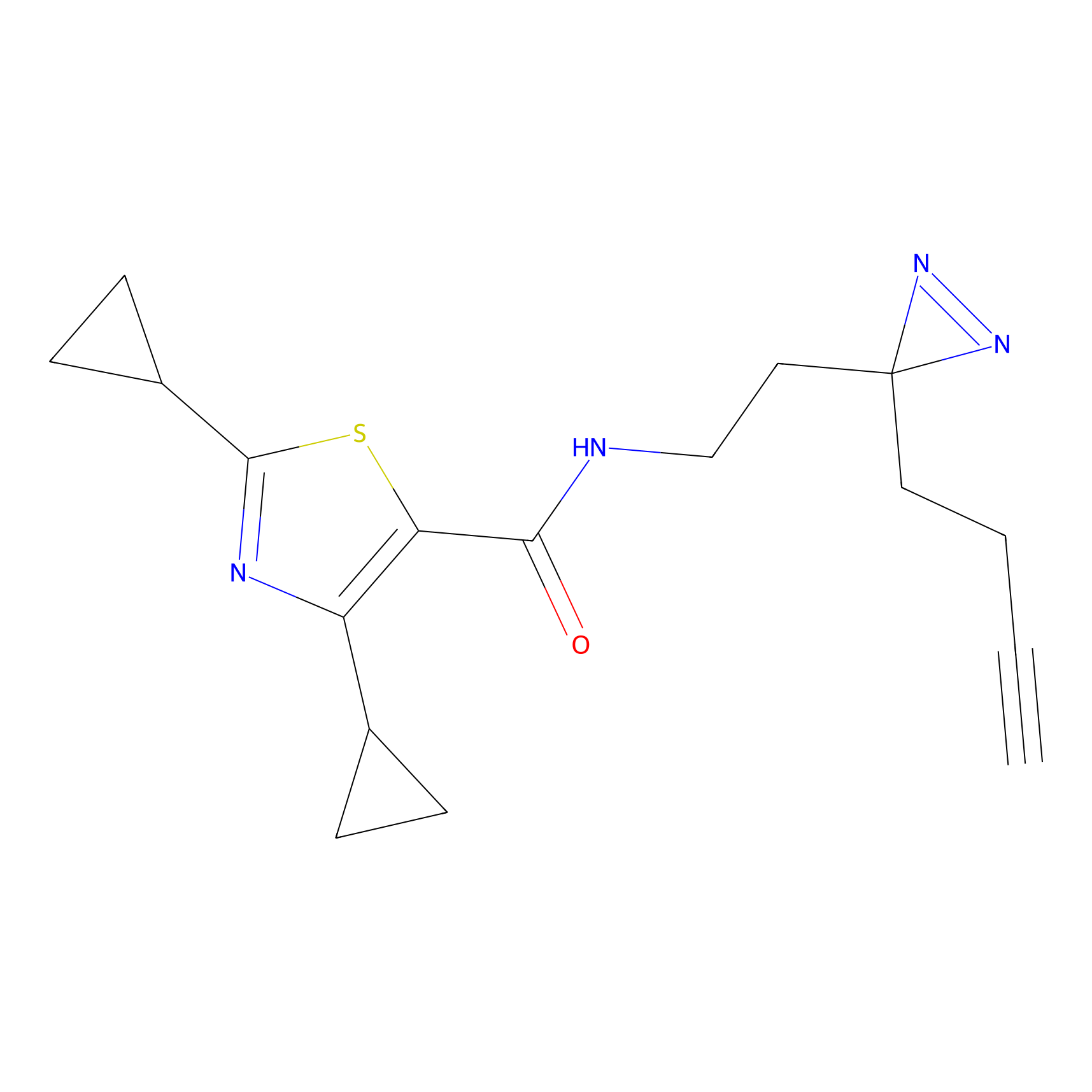
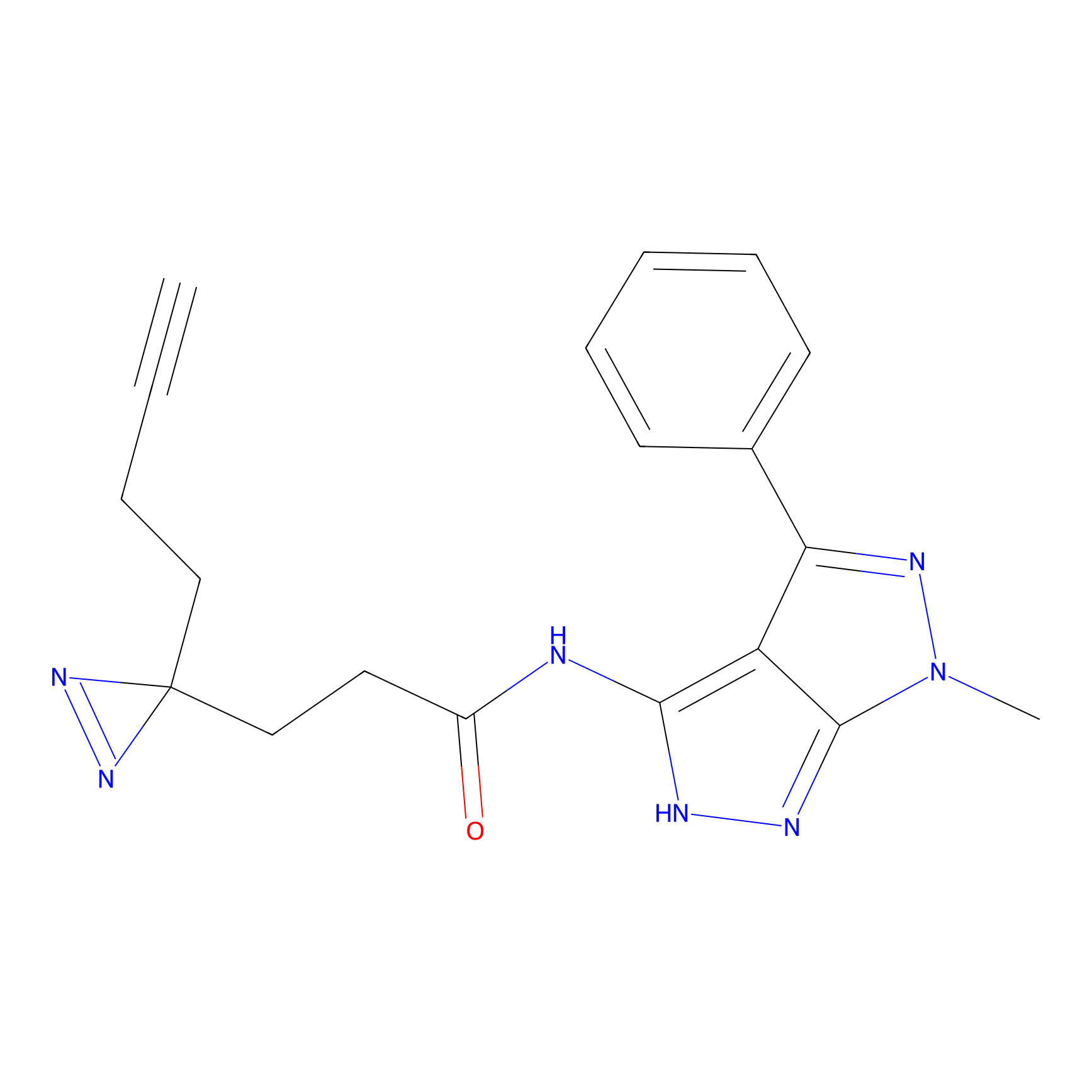
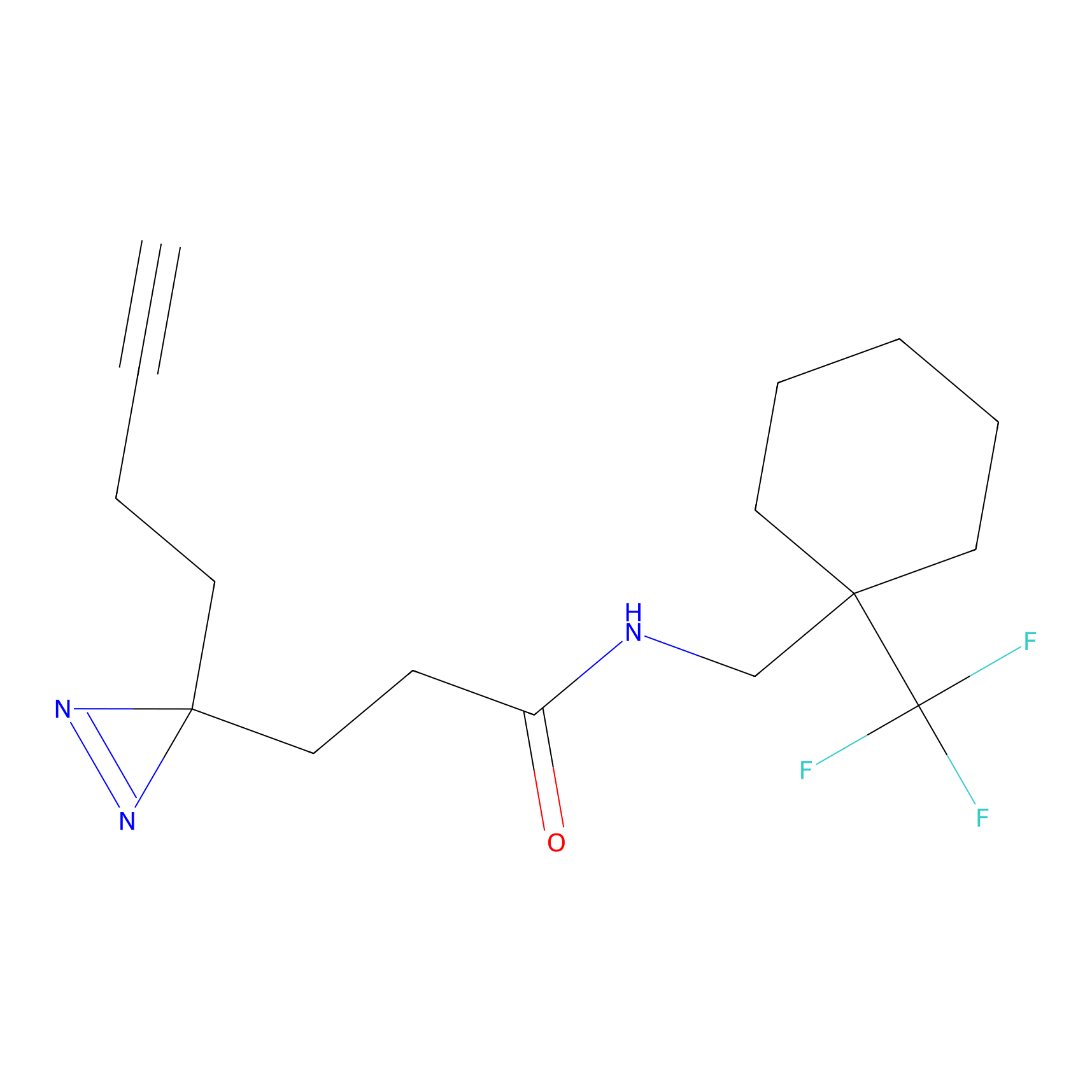
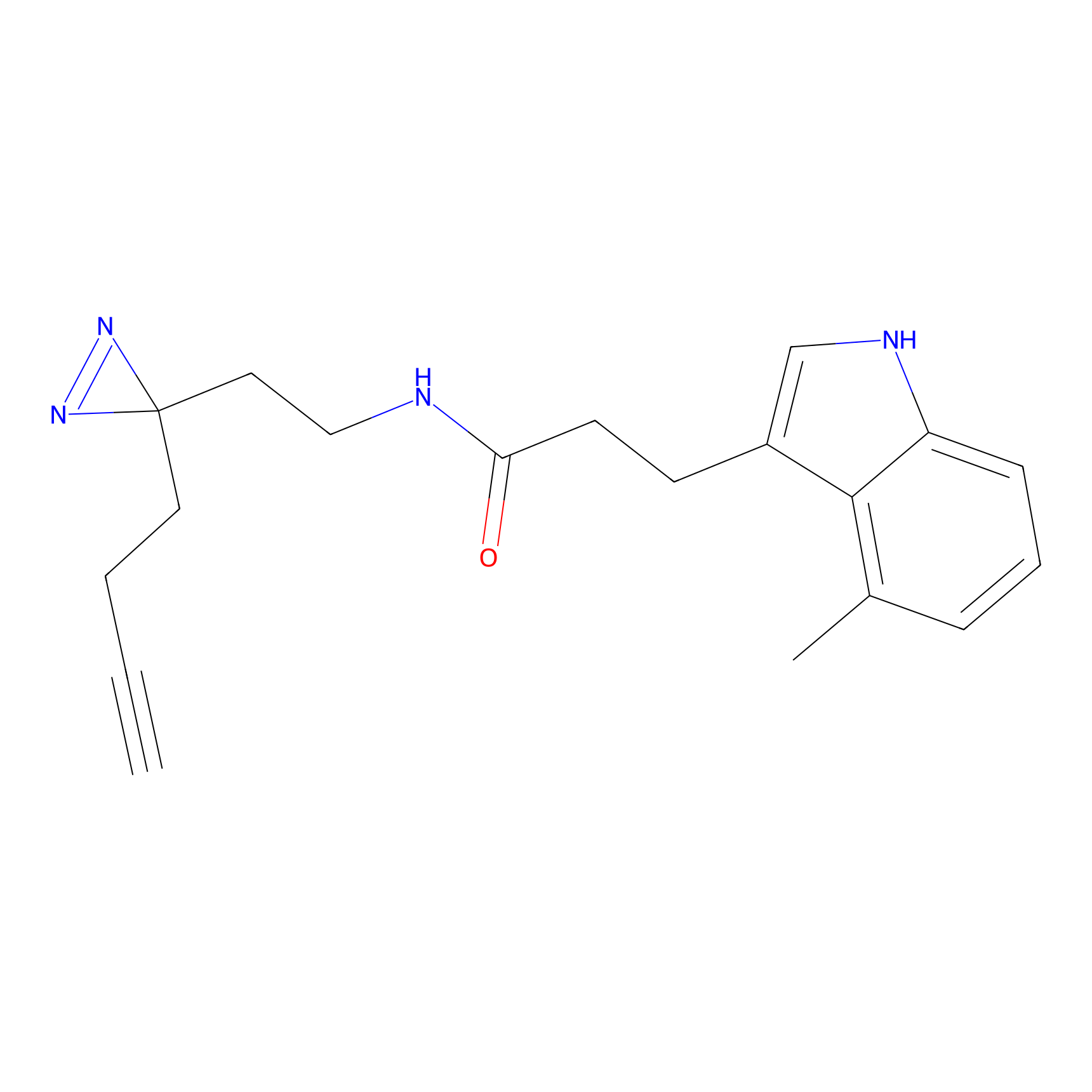
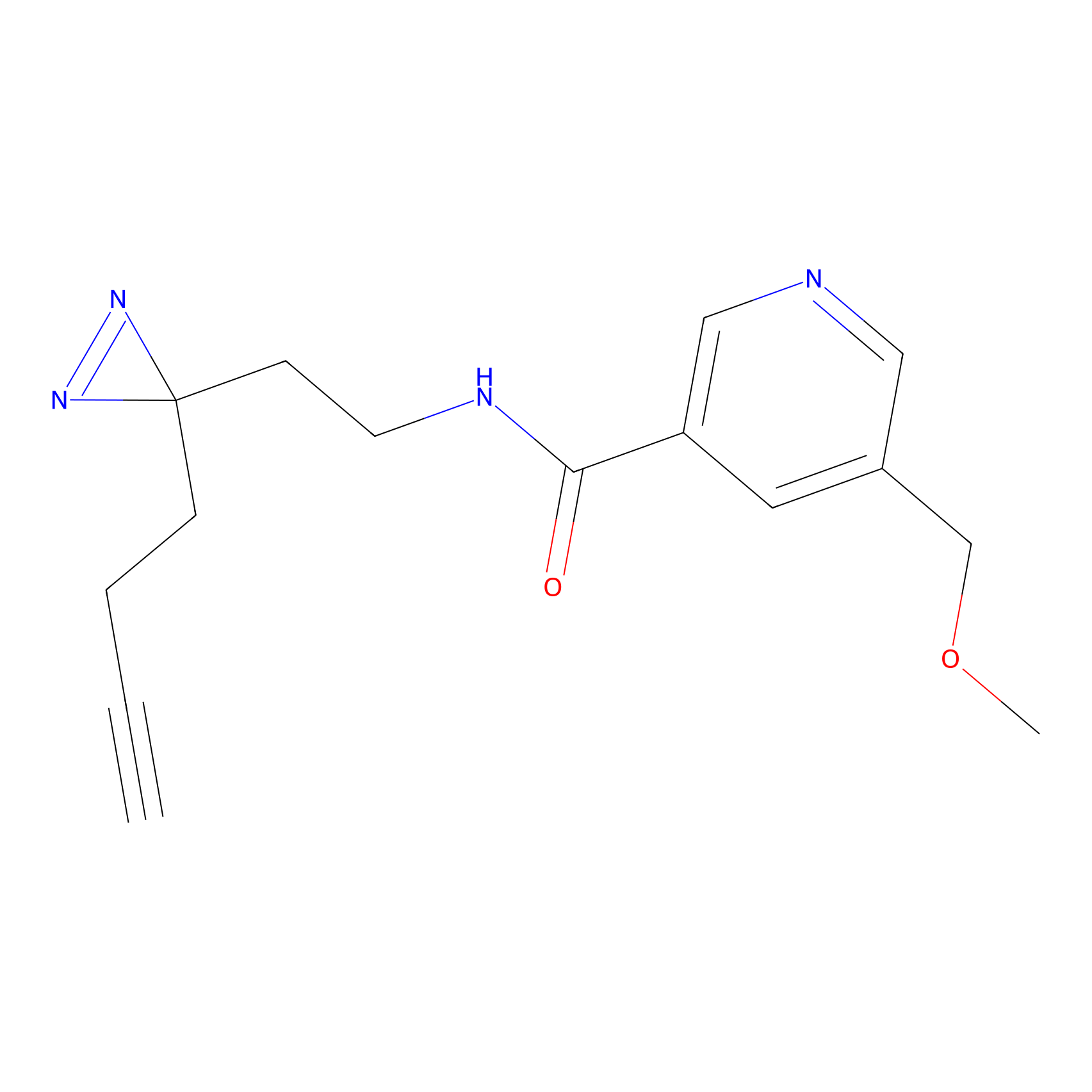
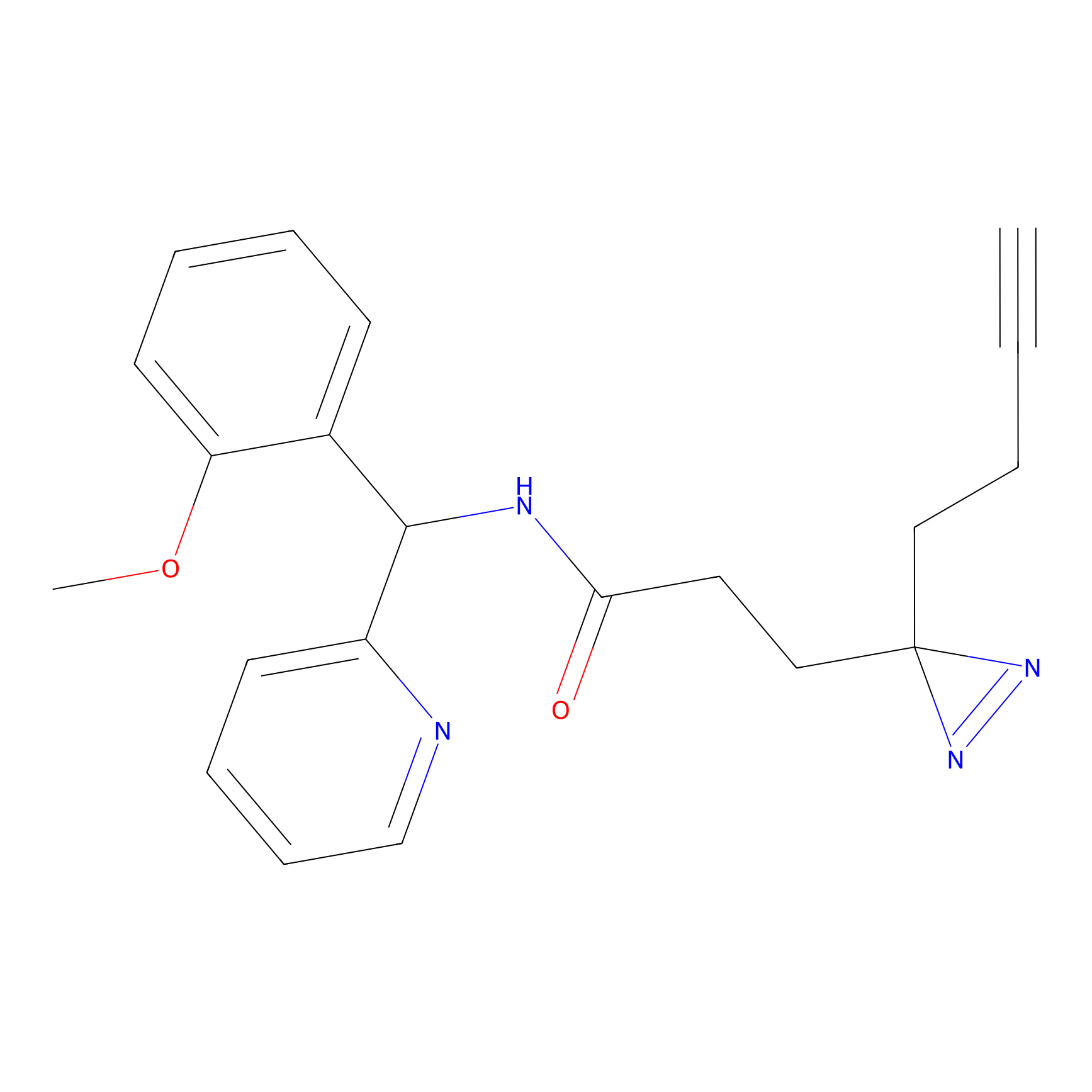
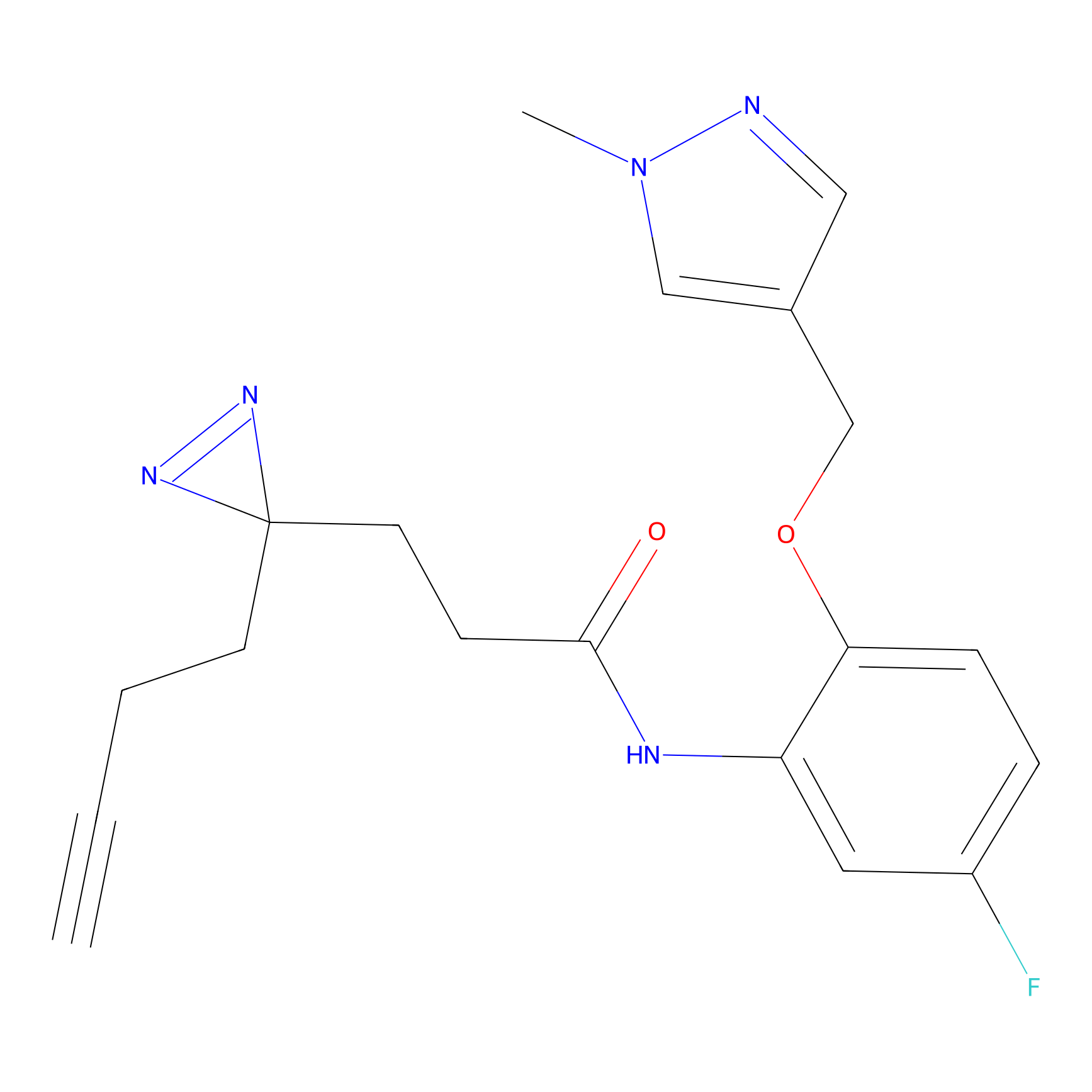
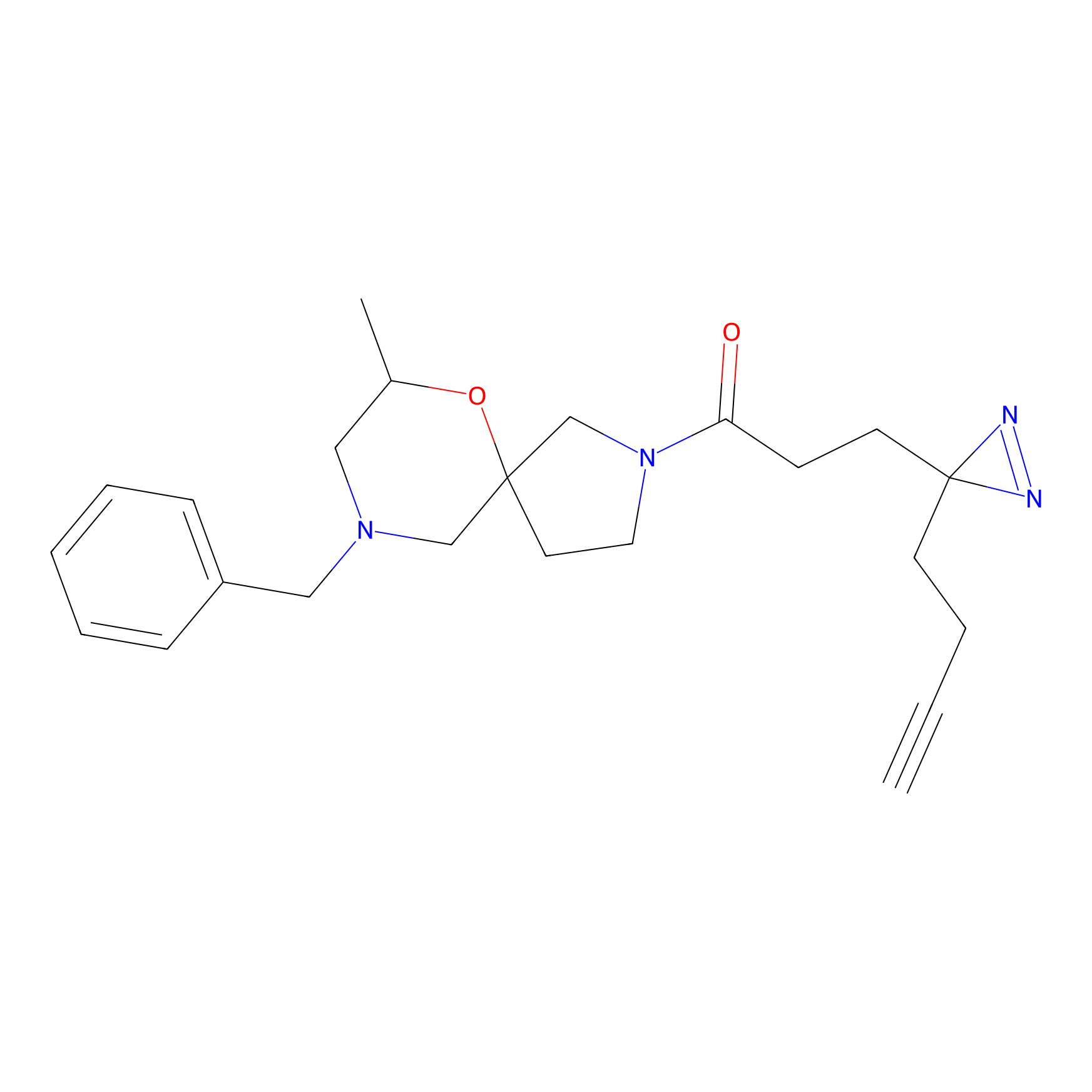
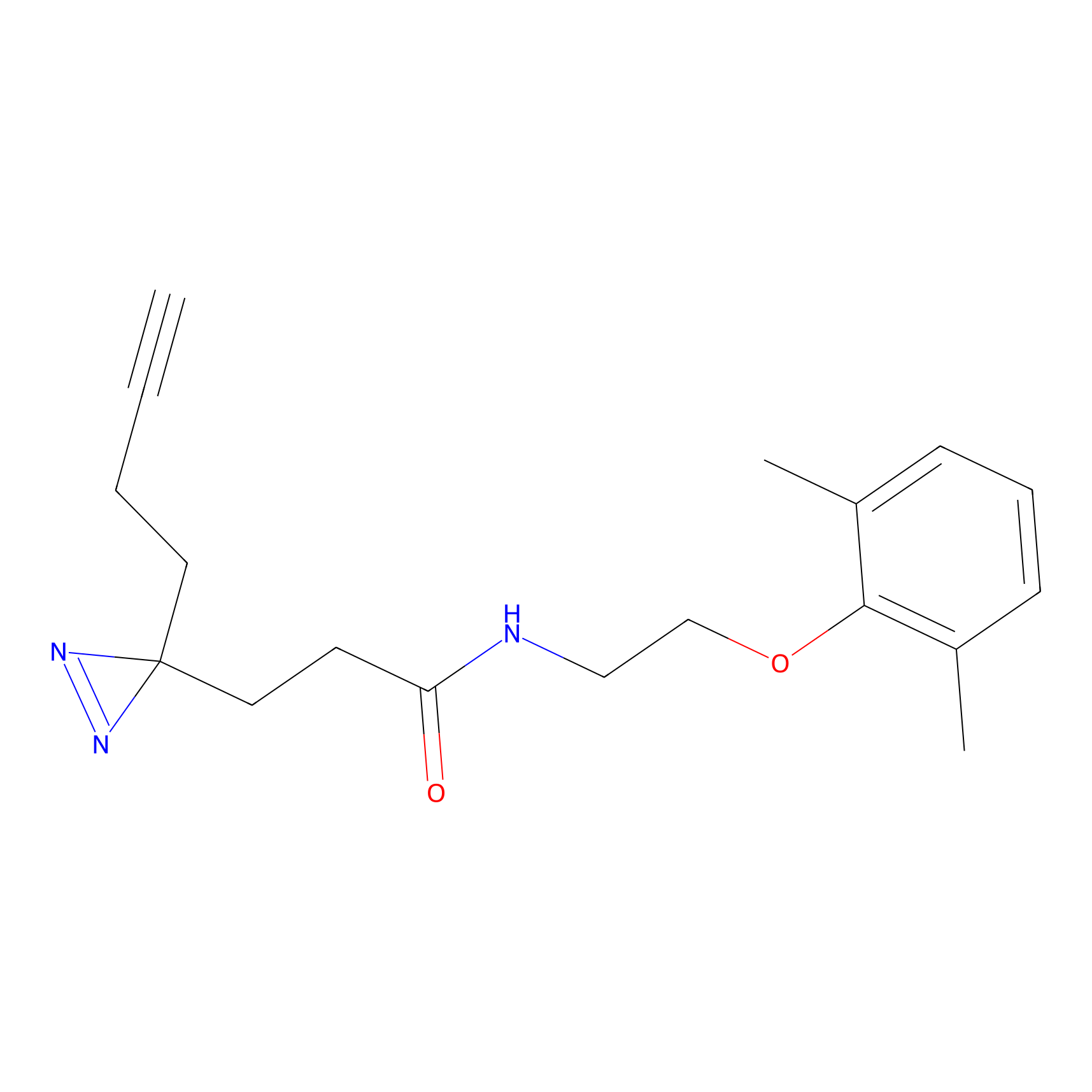
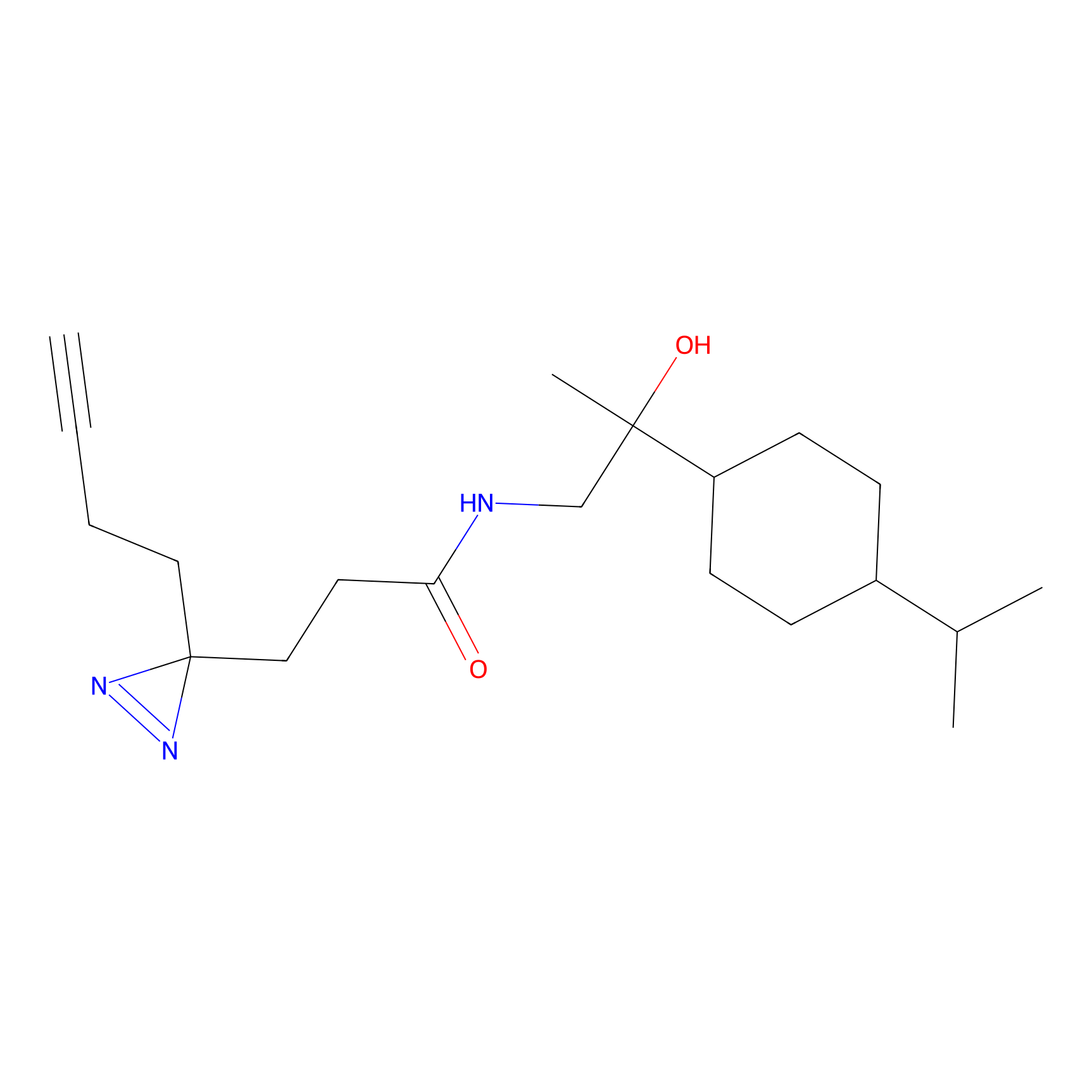
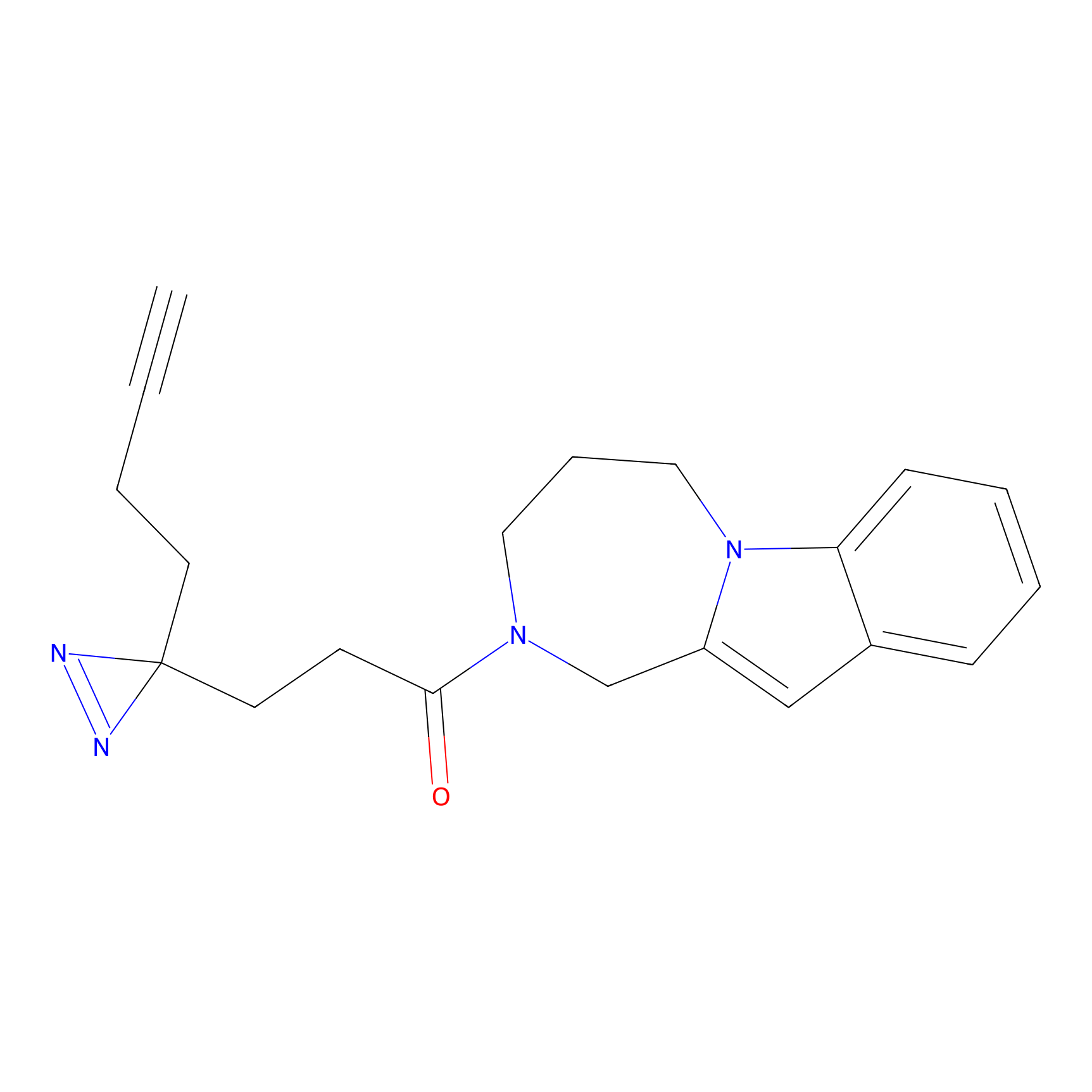
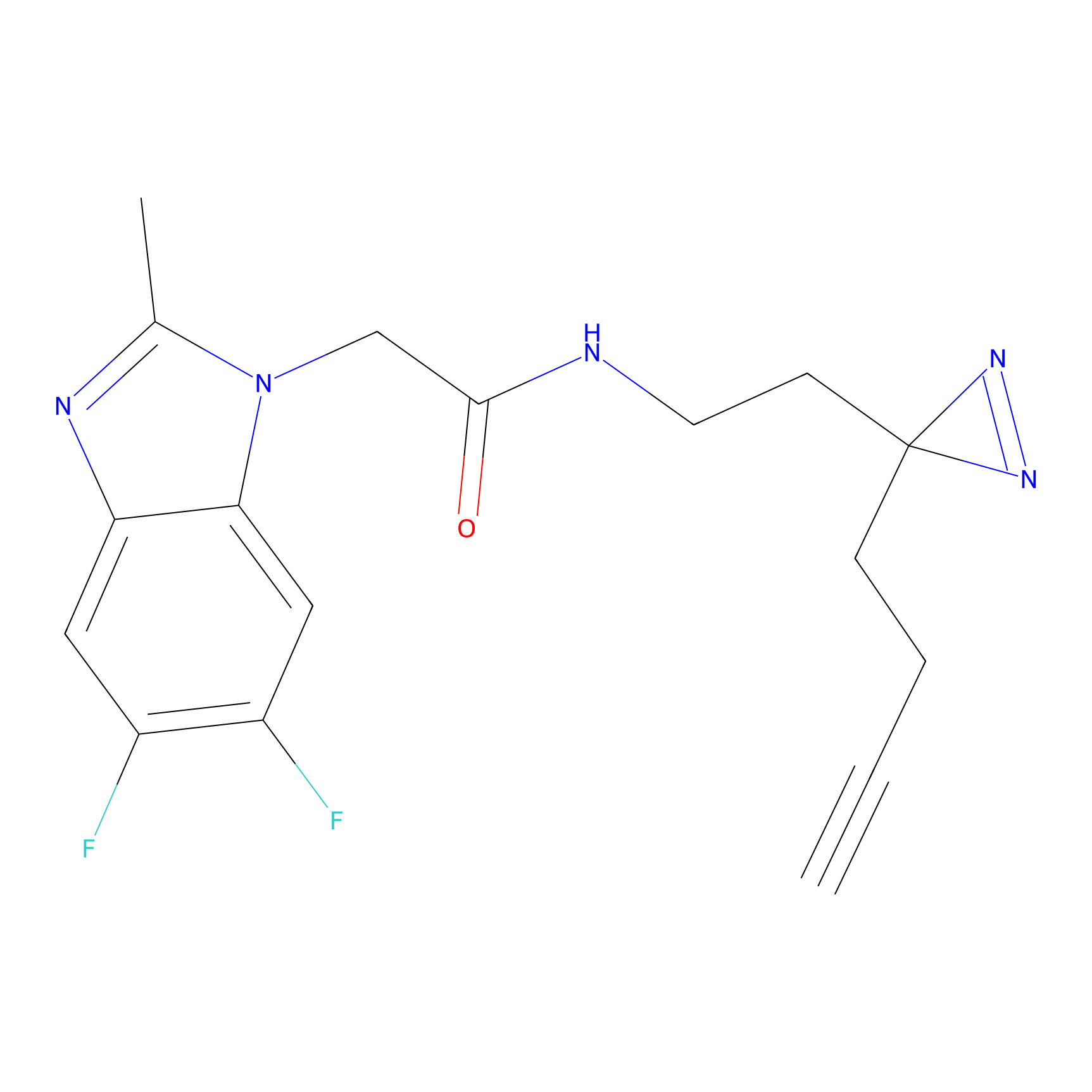
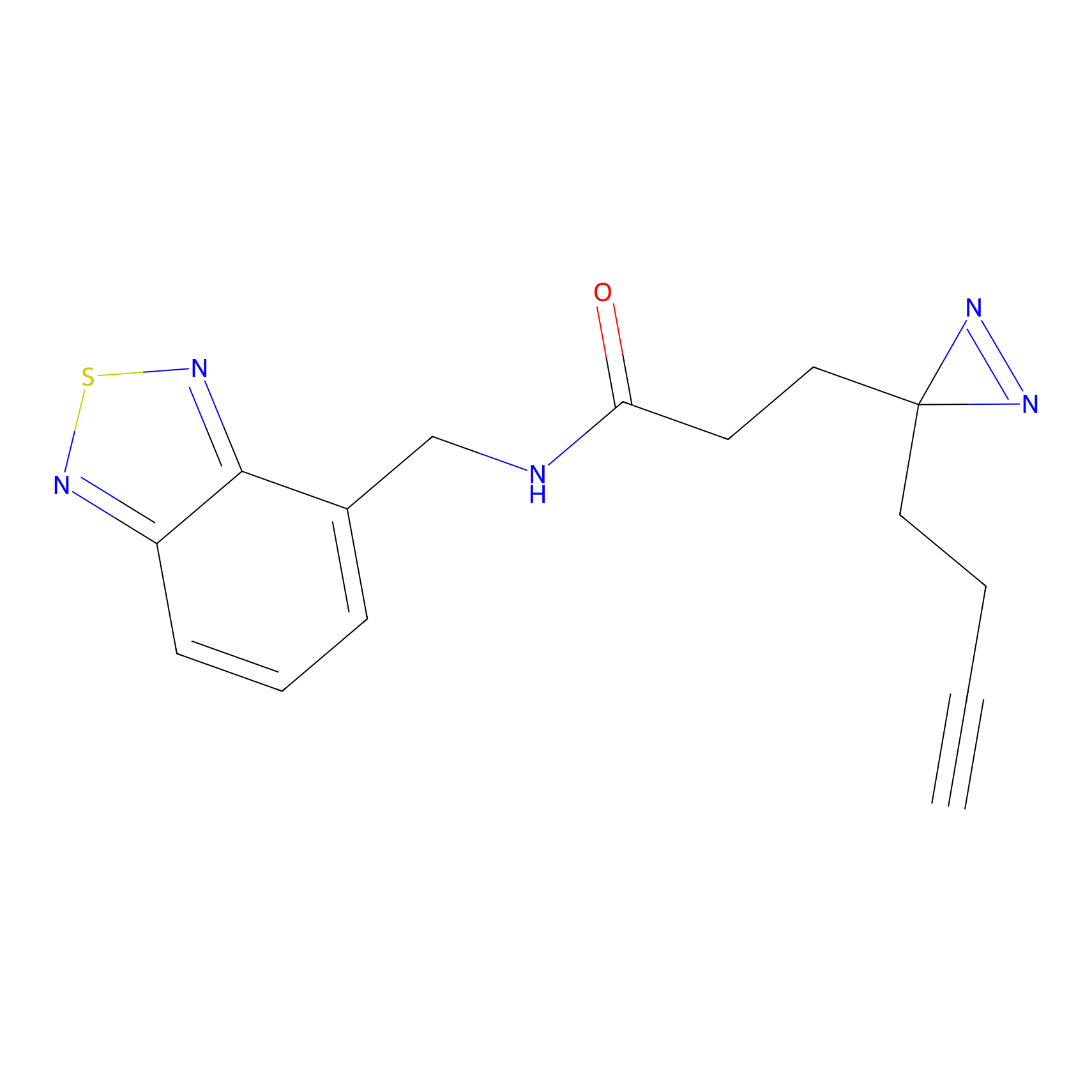
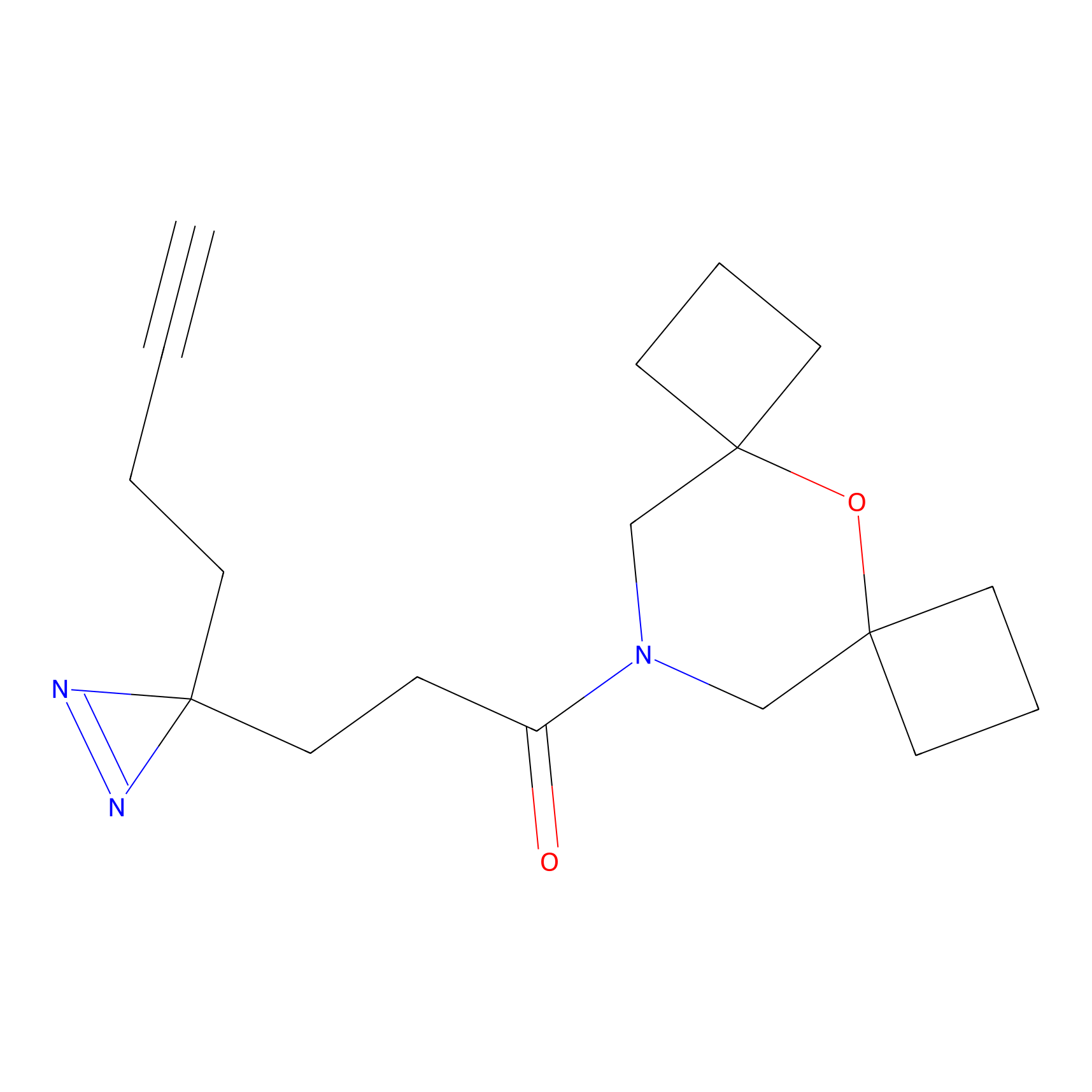
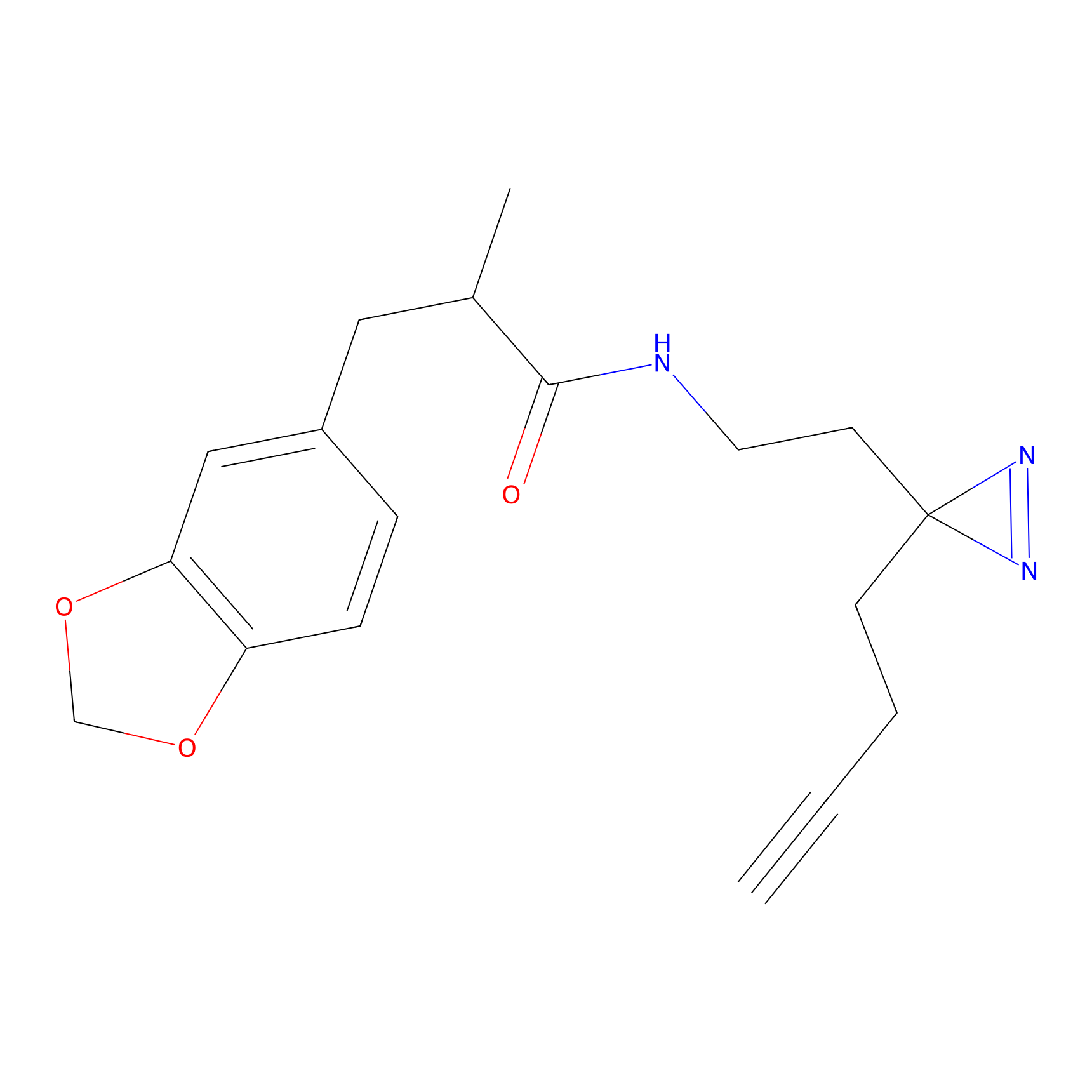
|
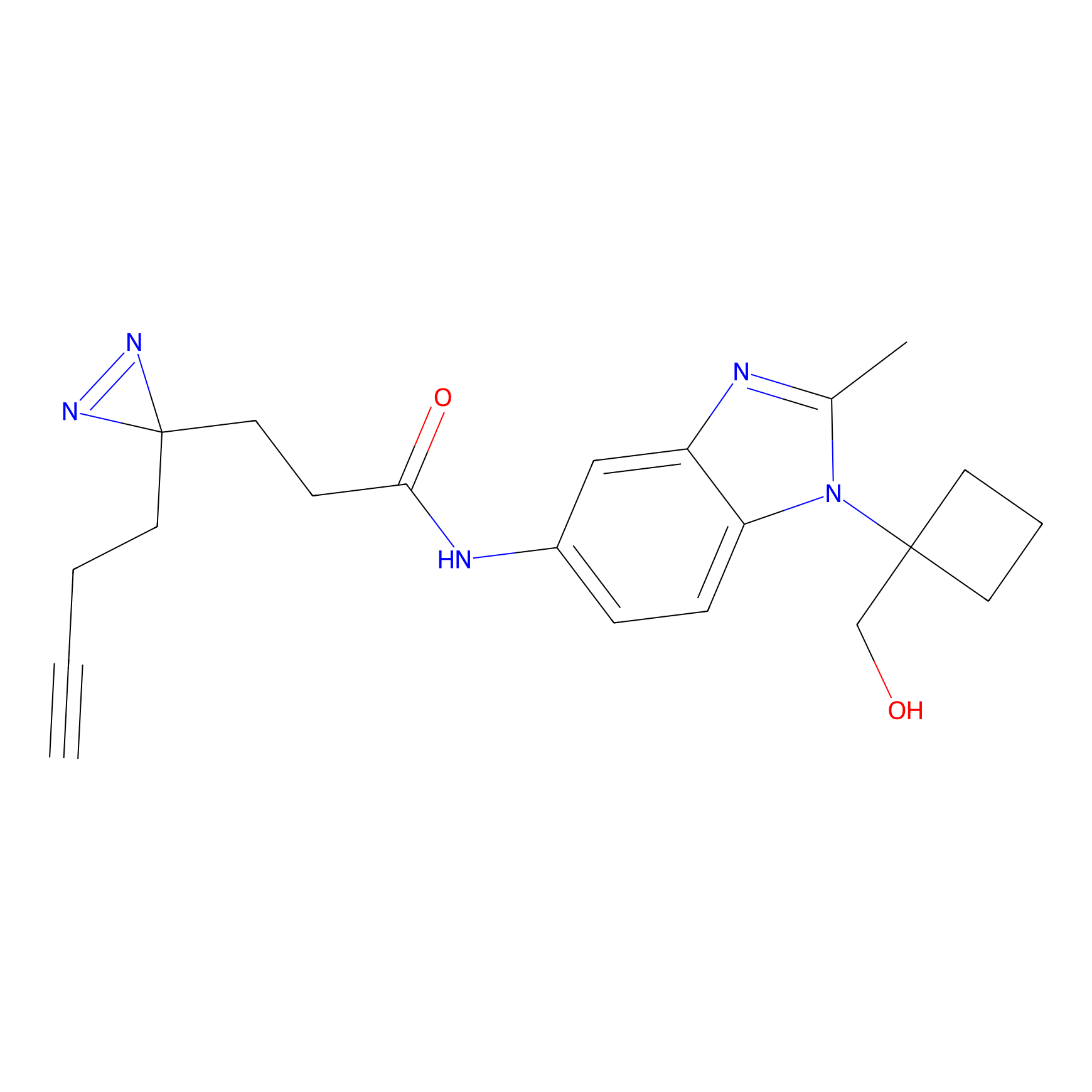
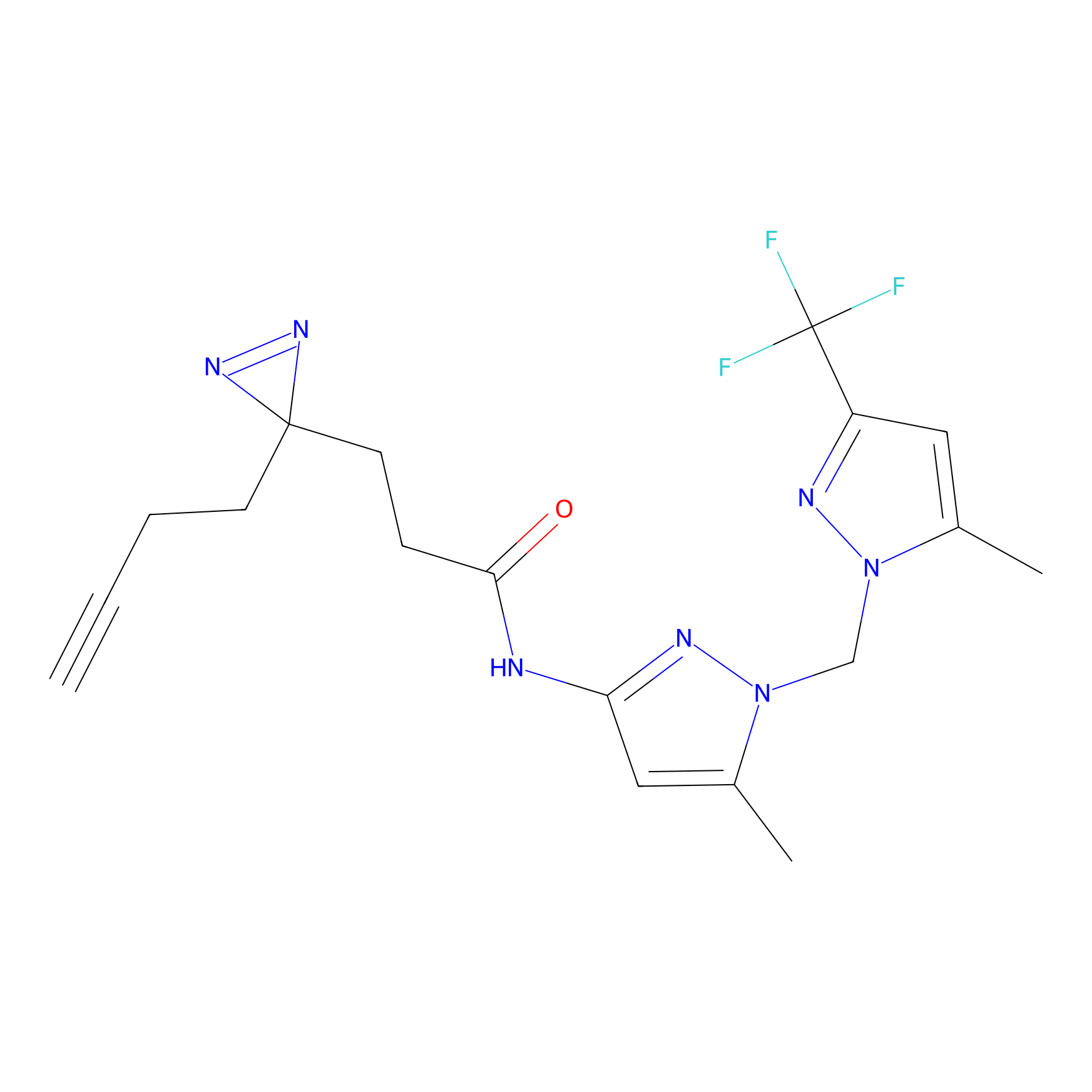
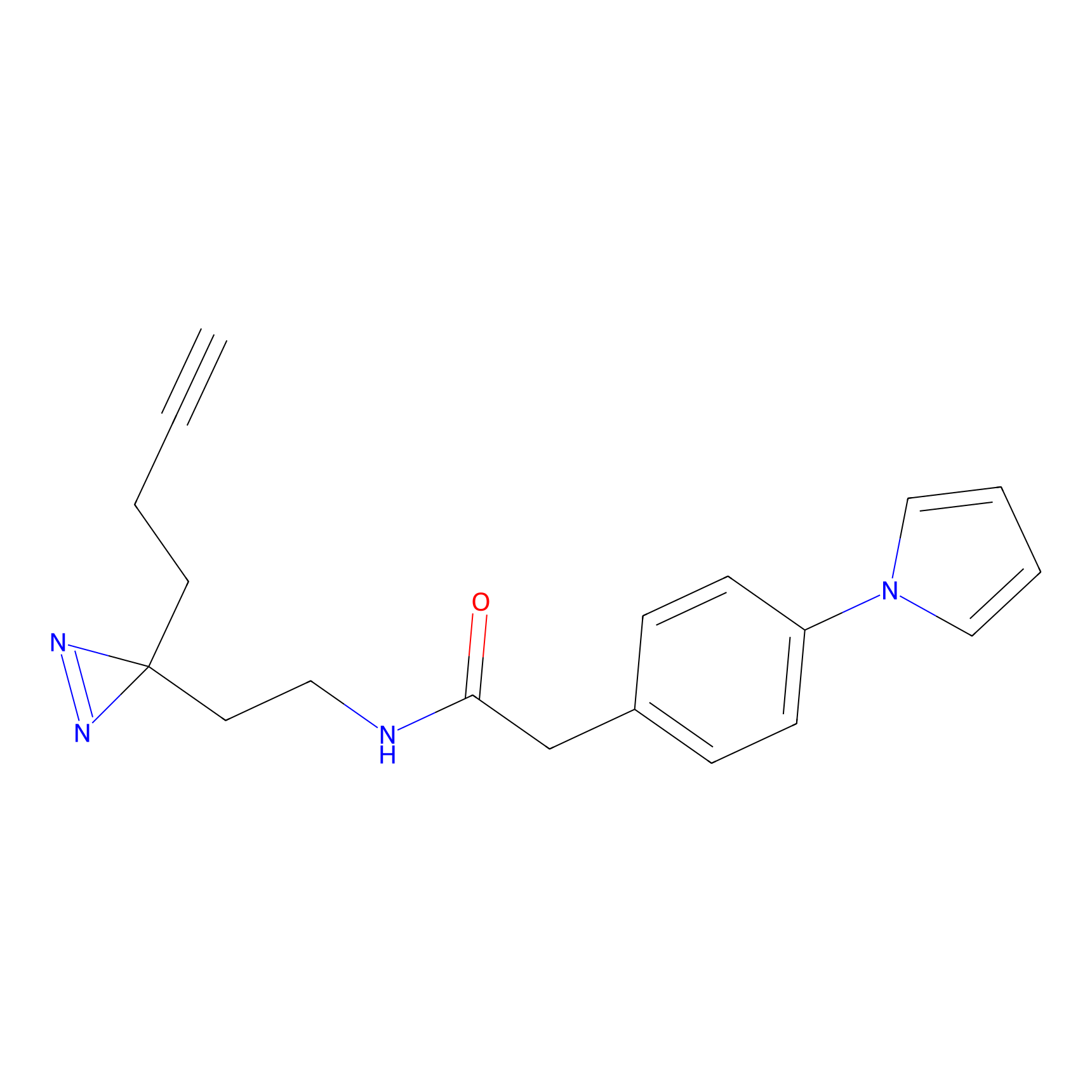
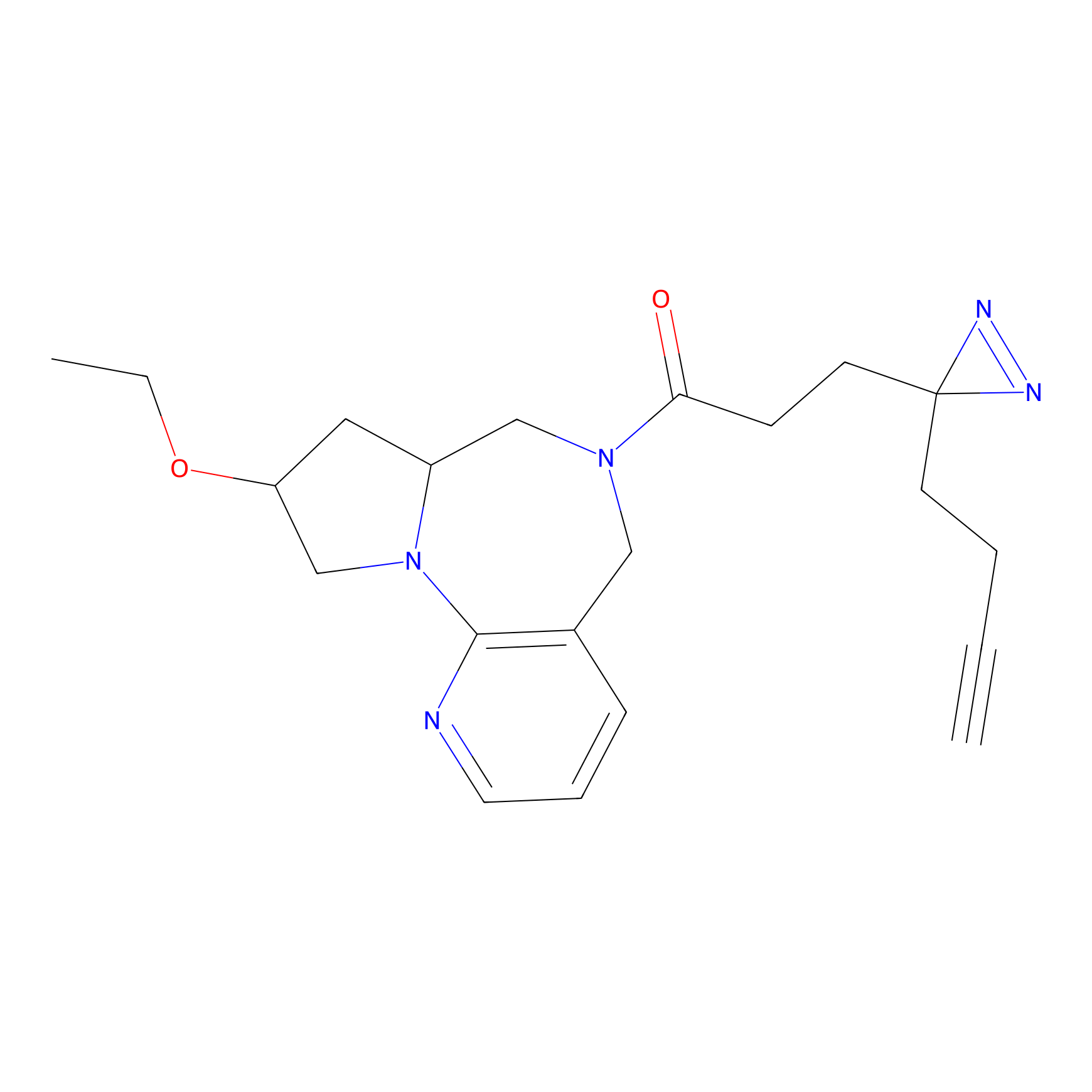
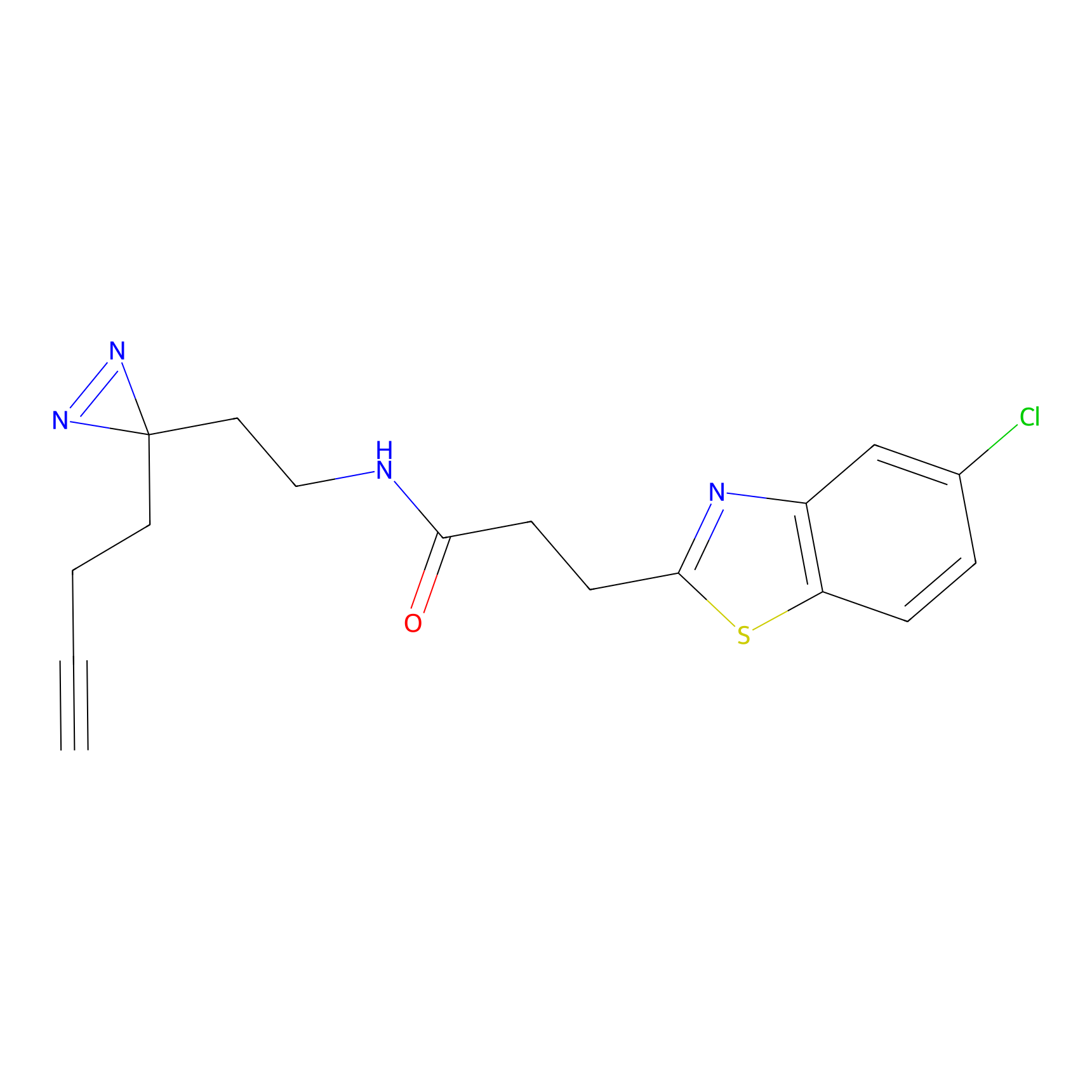
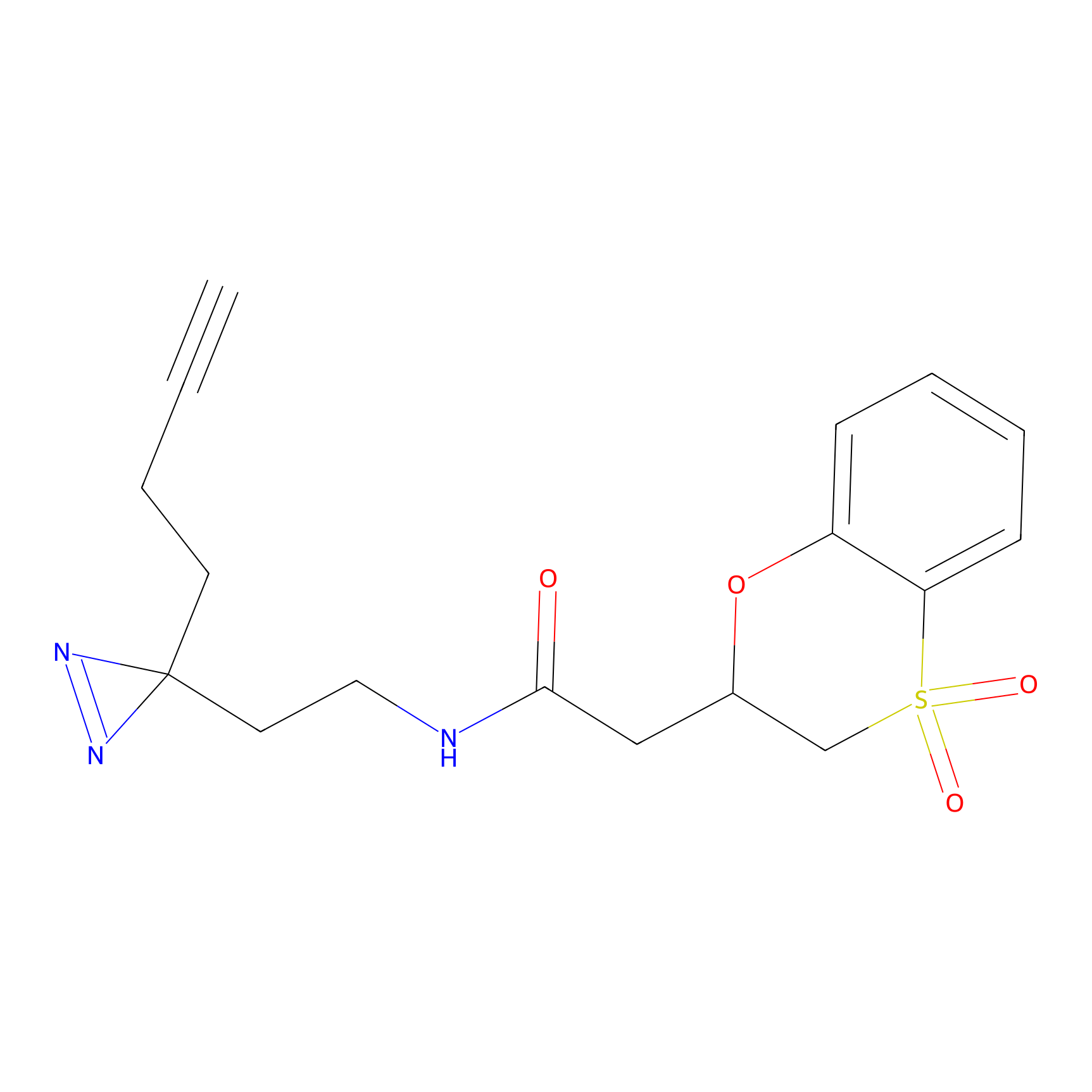
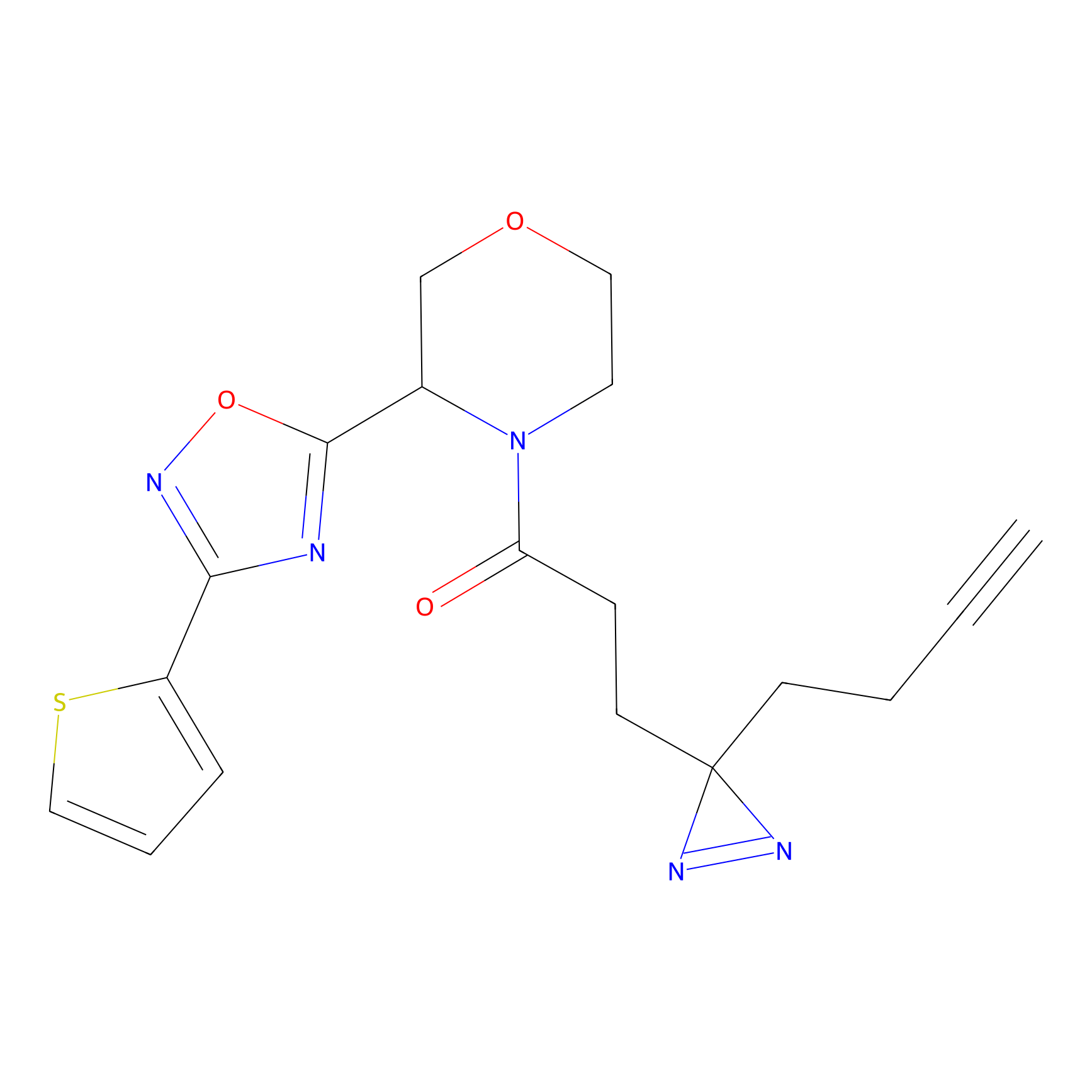
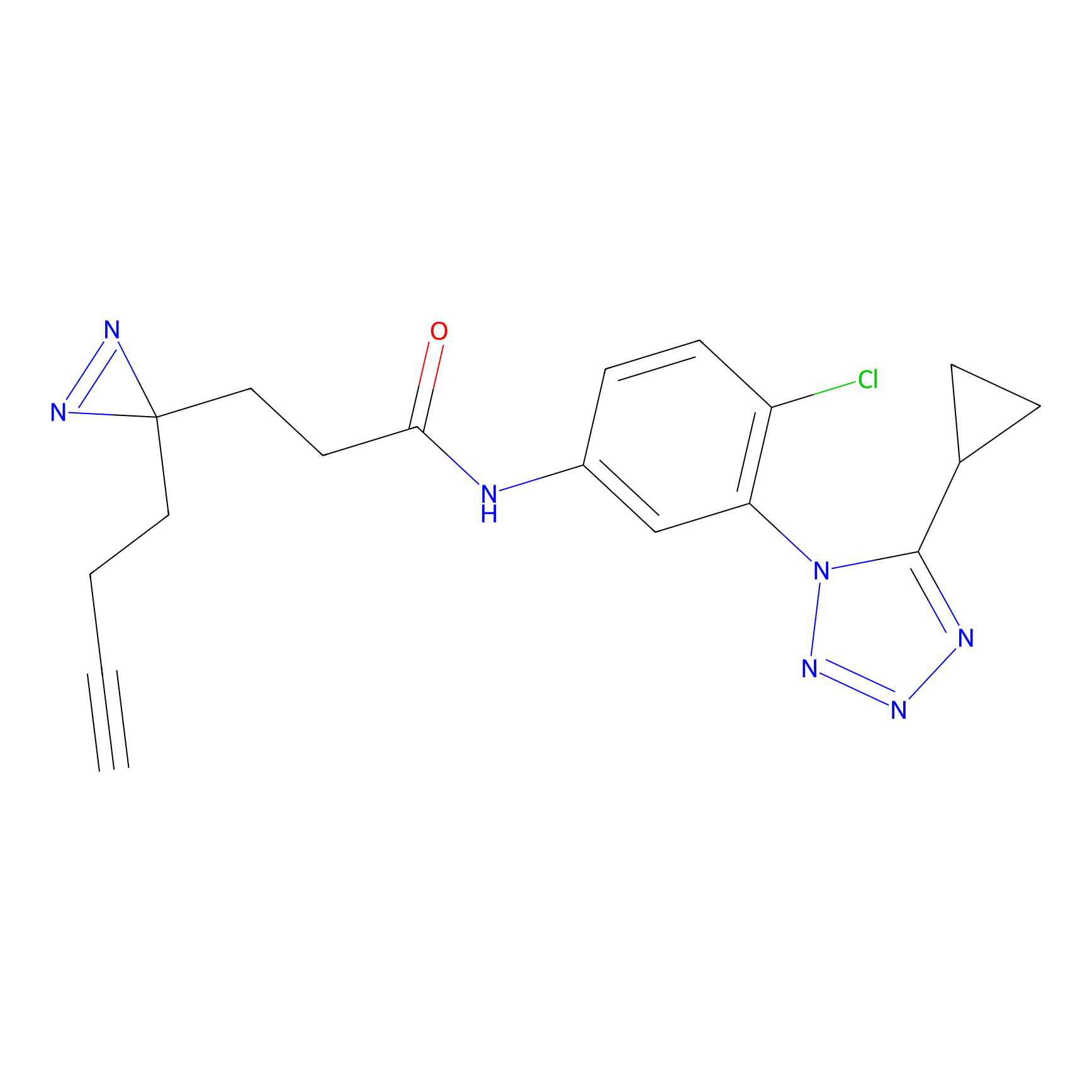
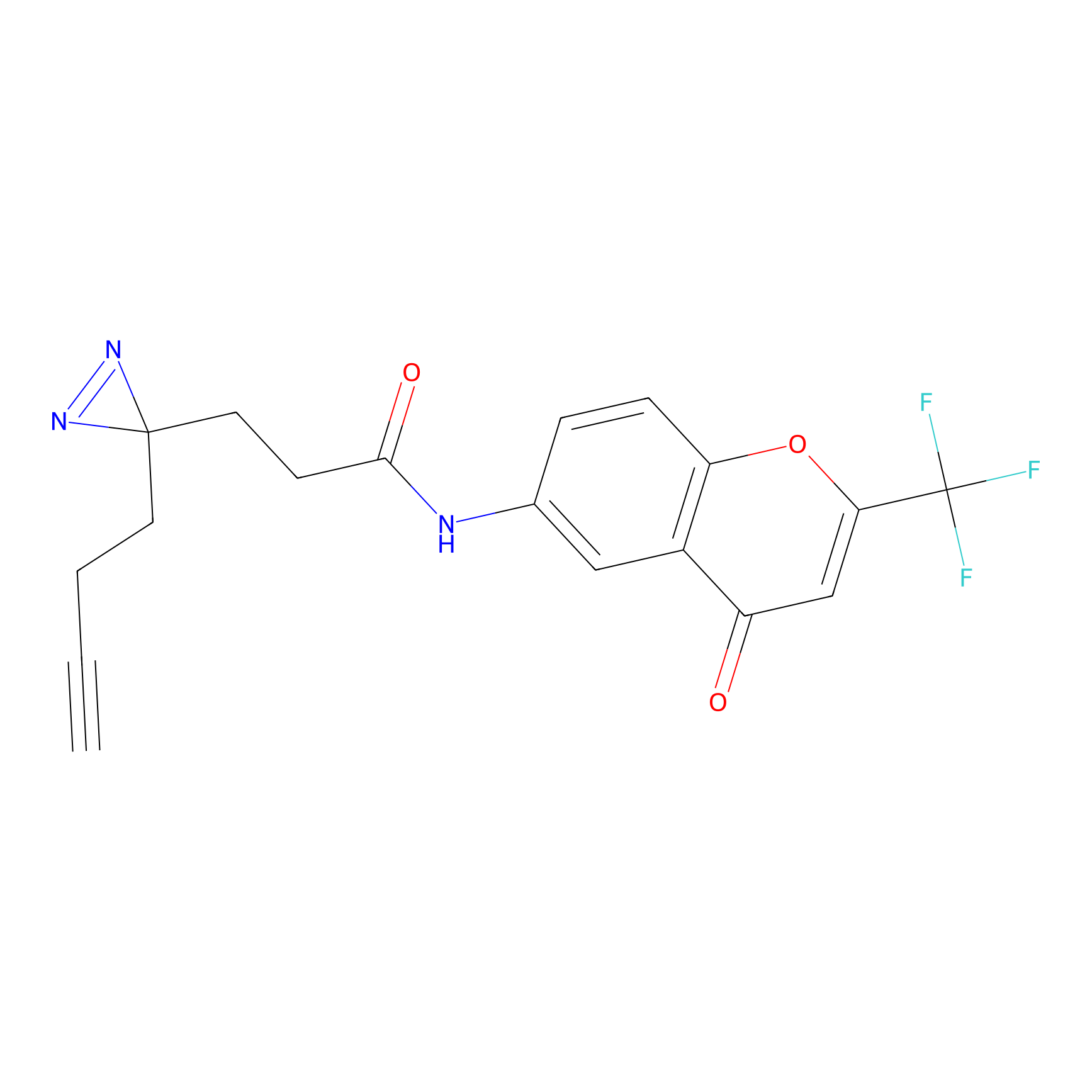
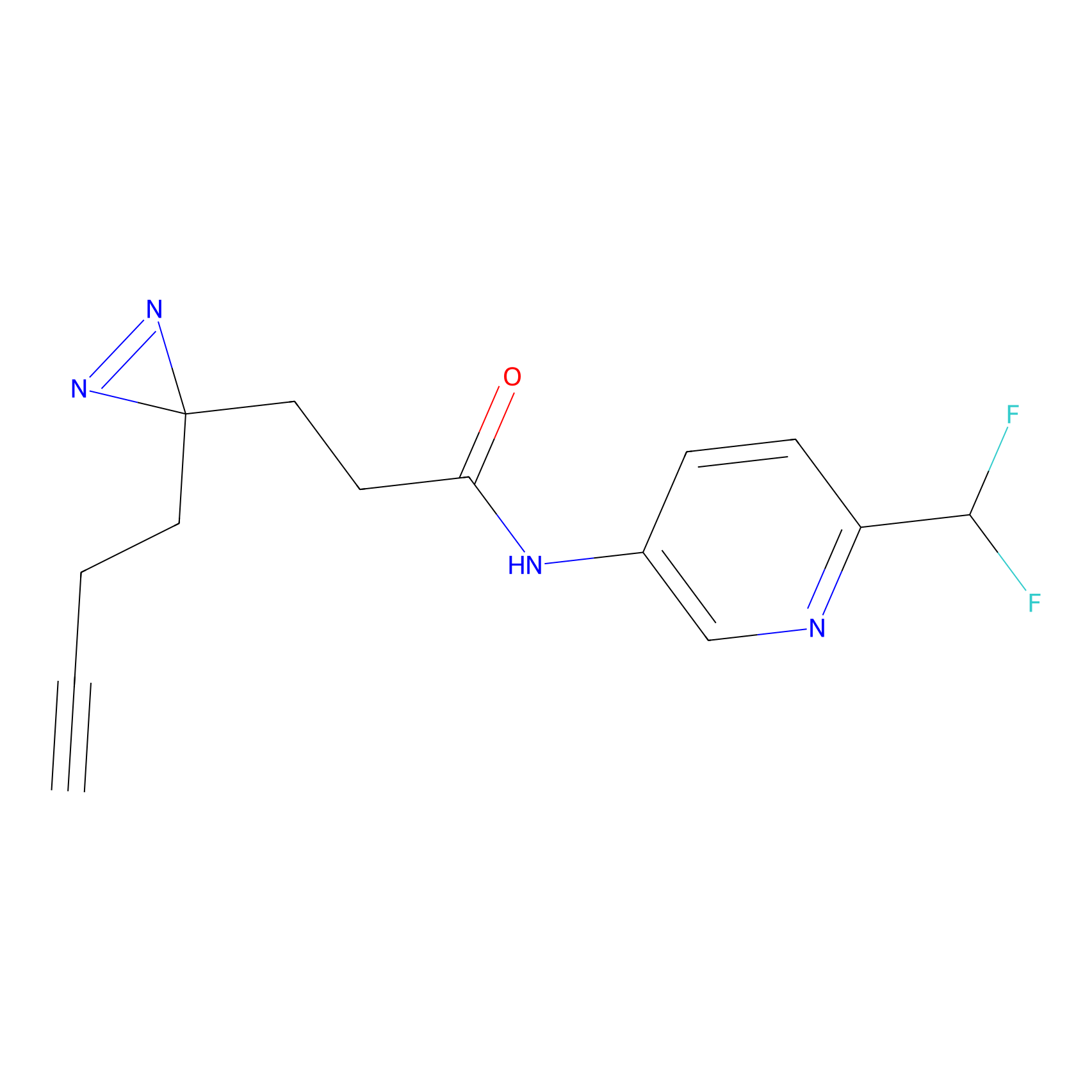
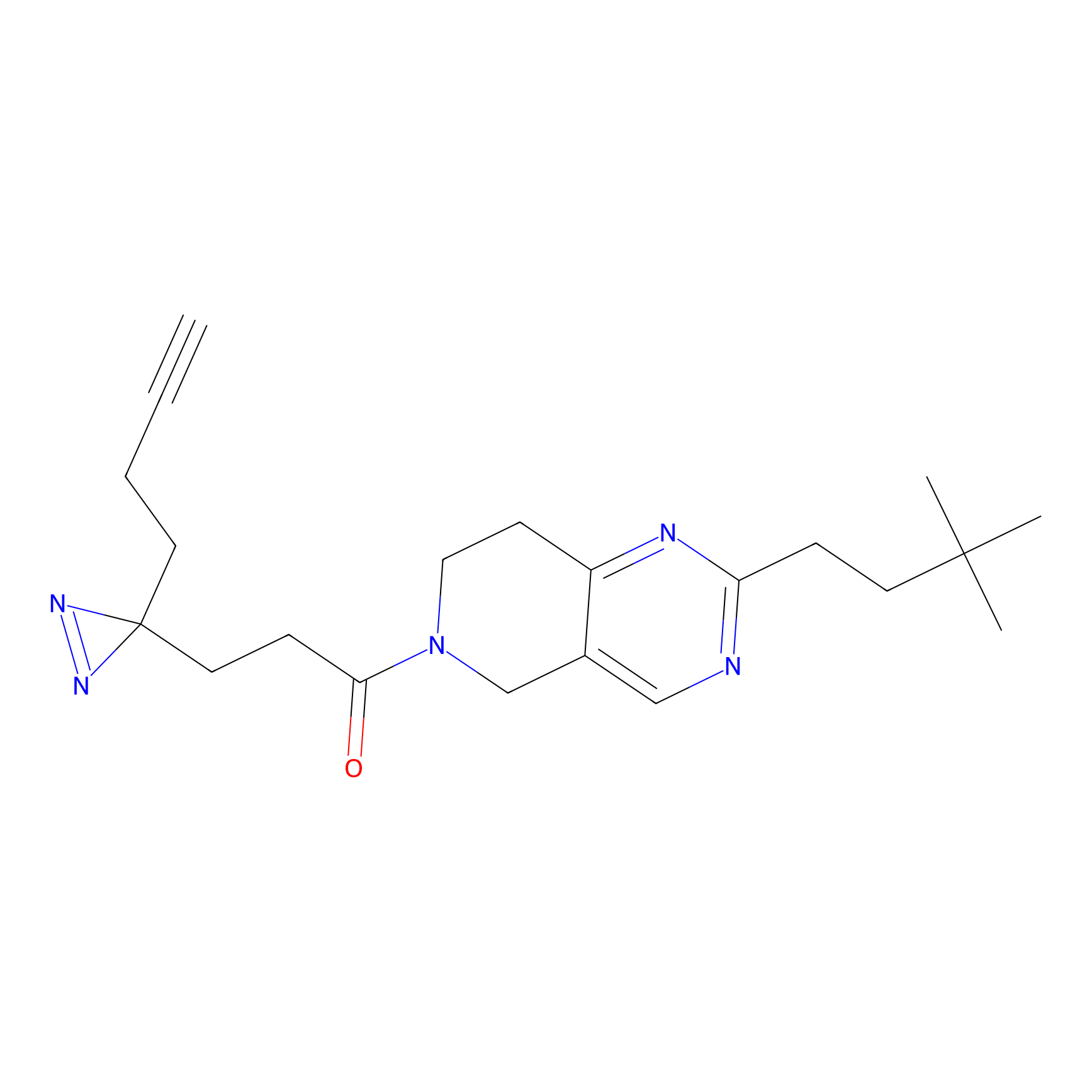
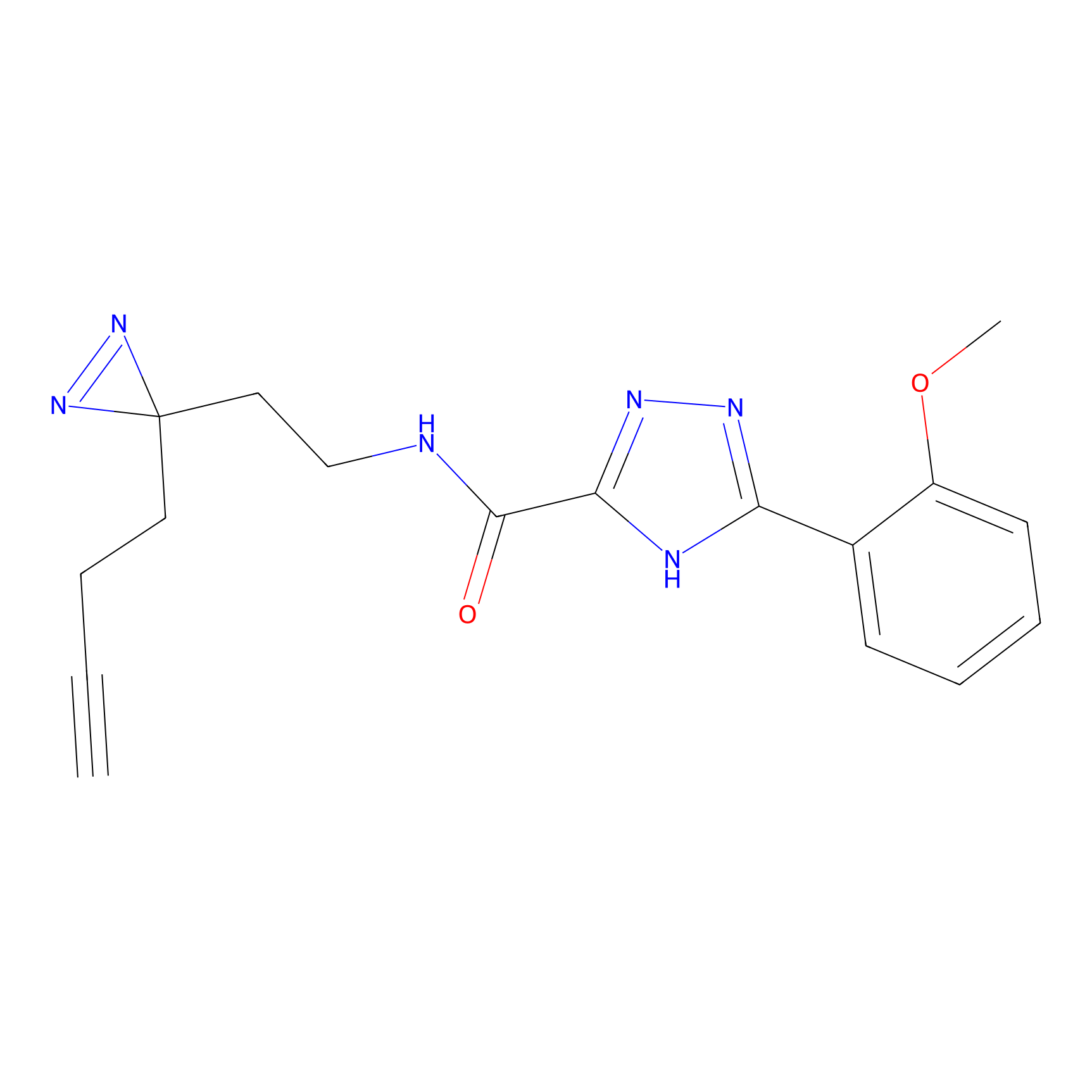
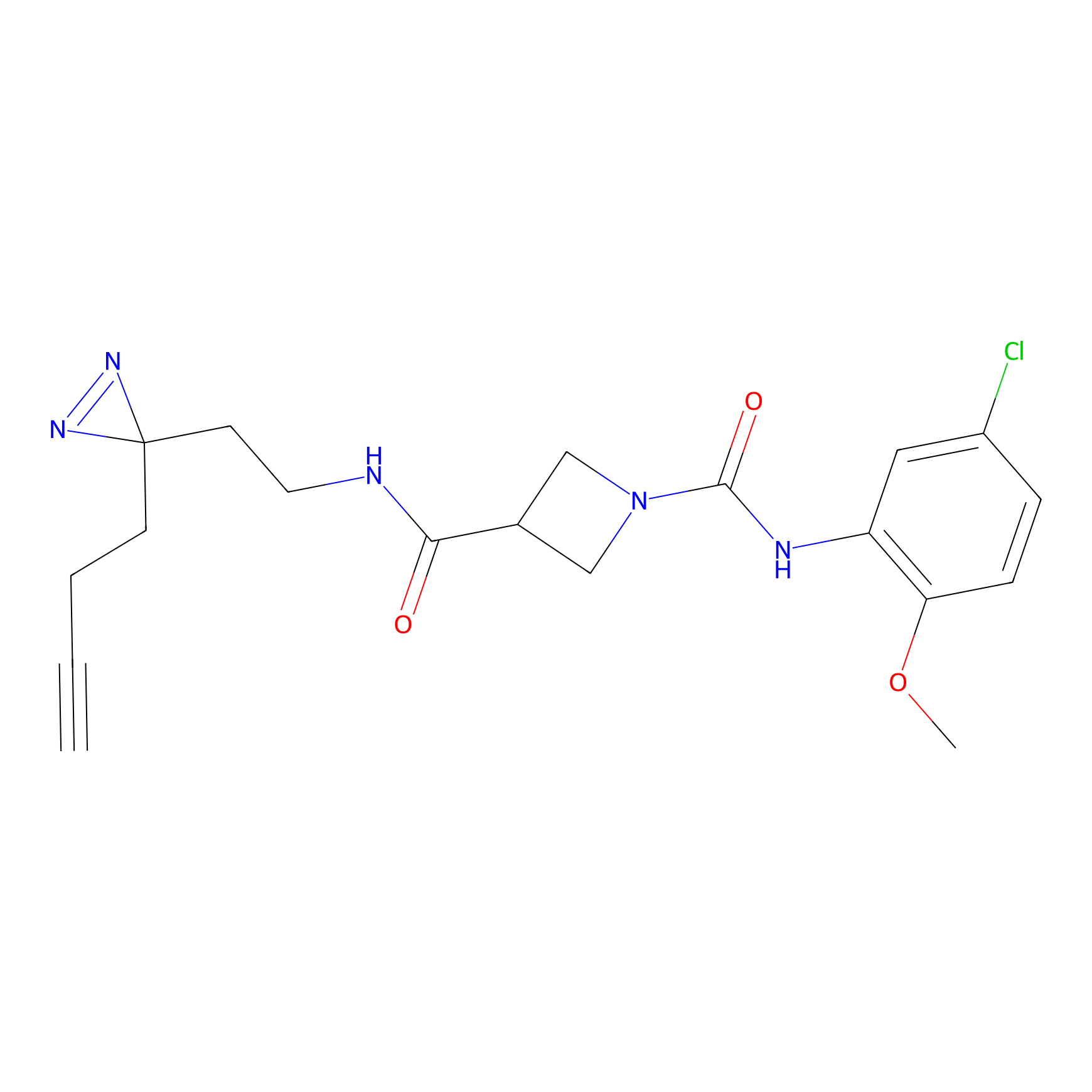
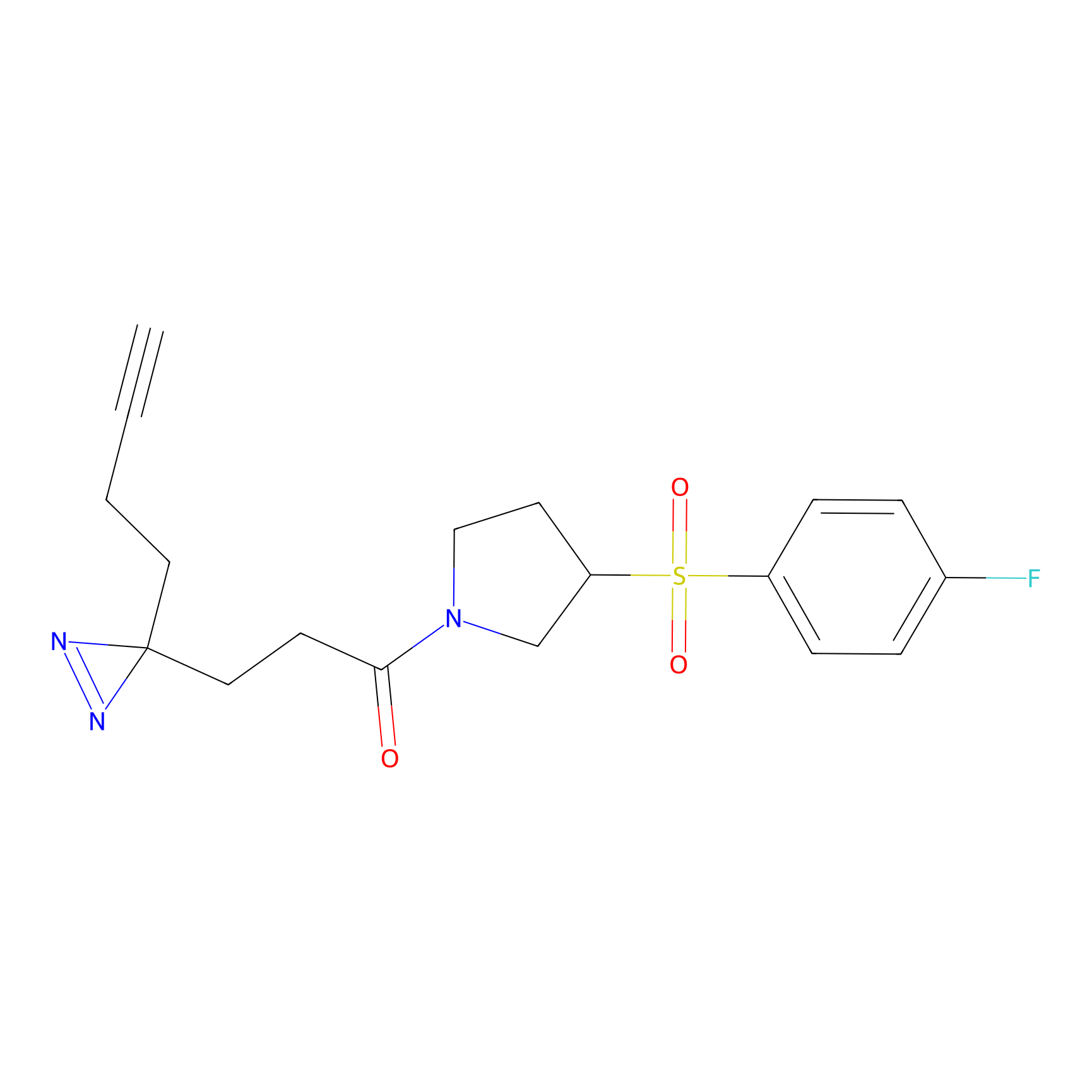
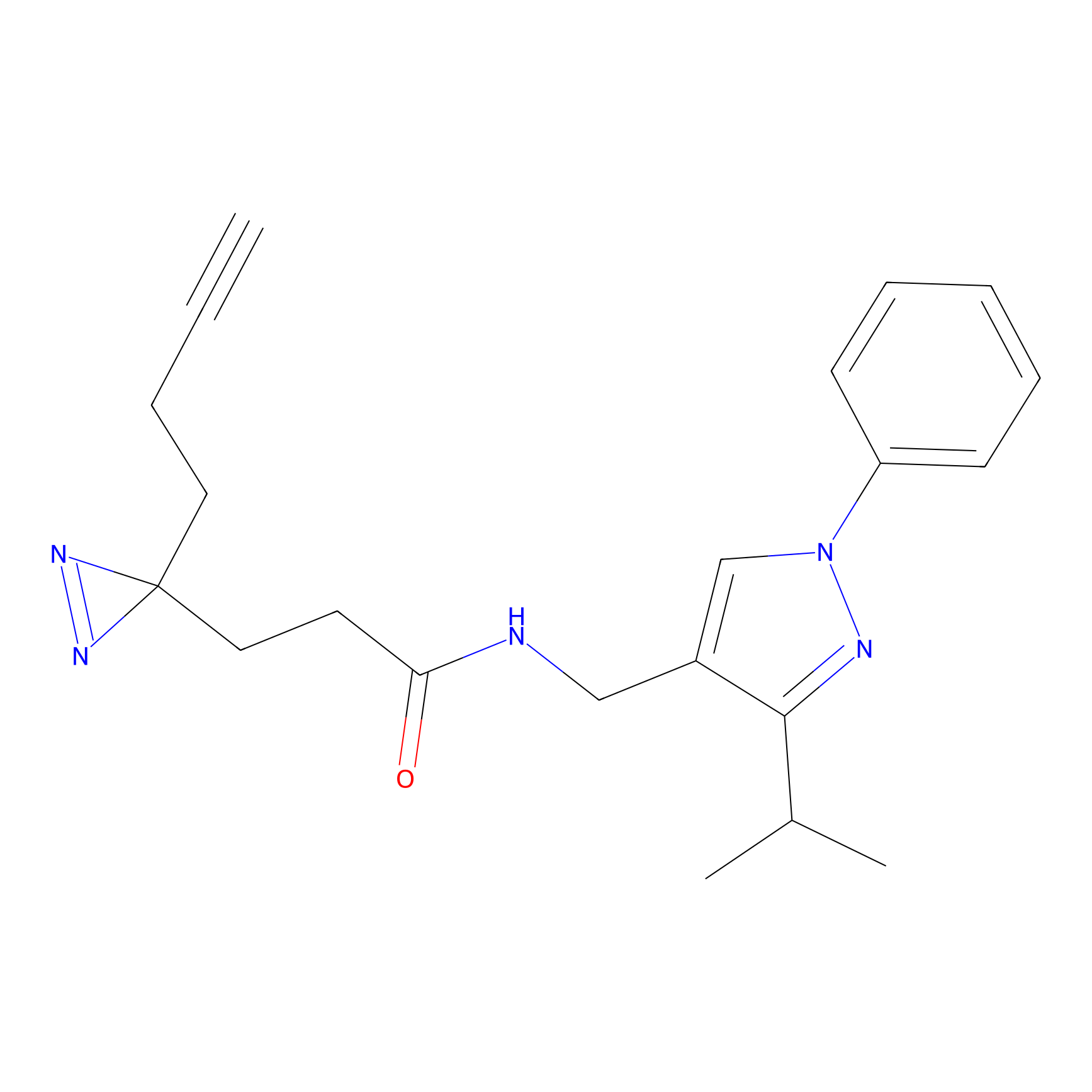
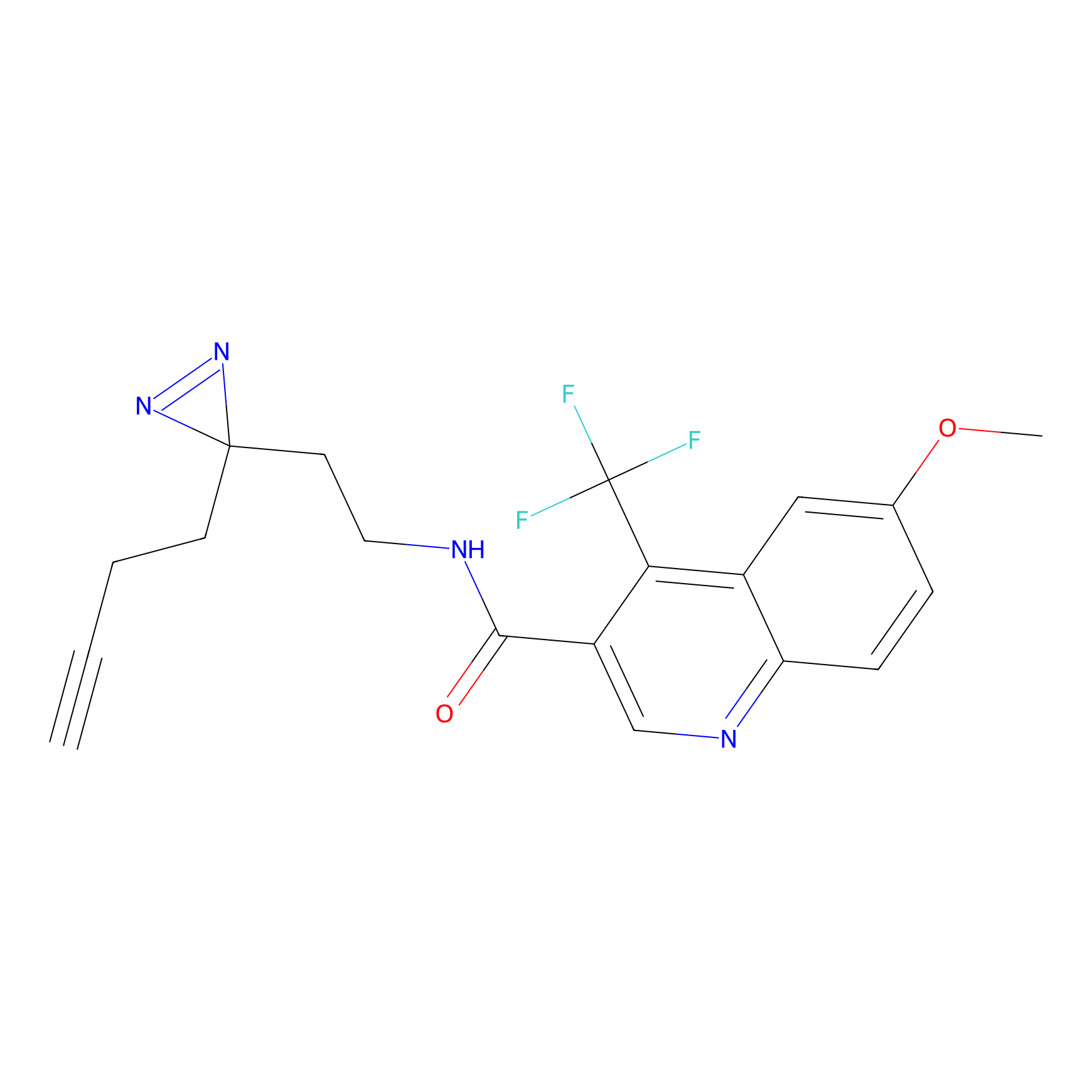
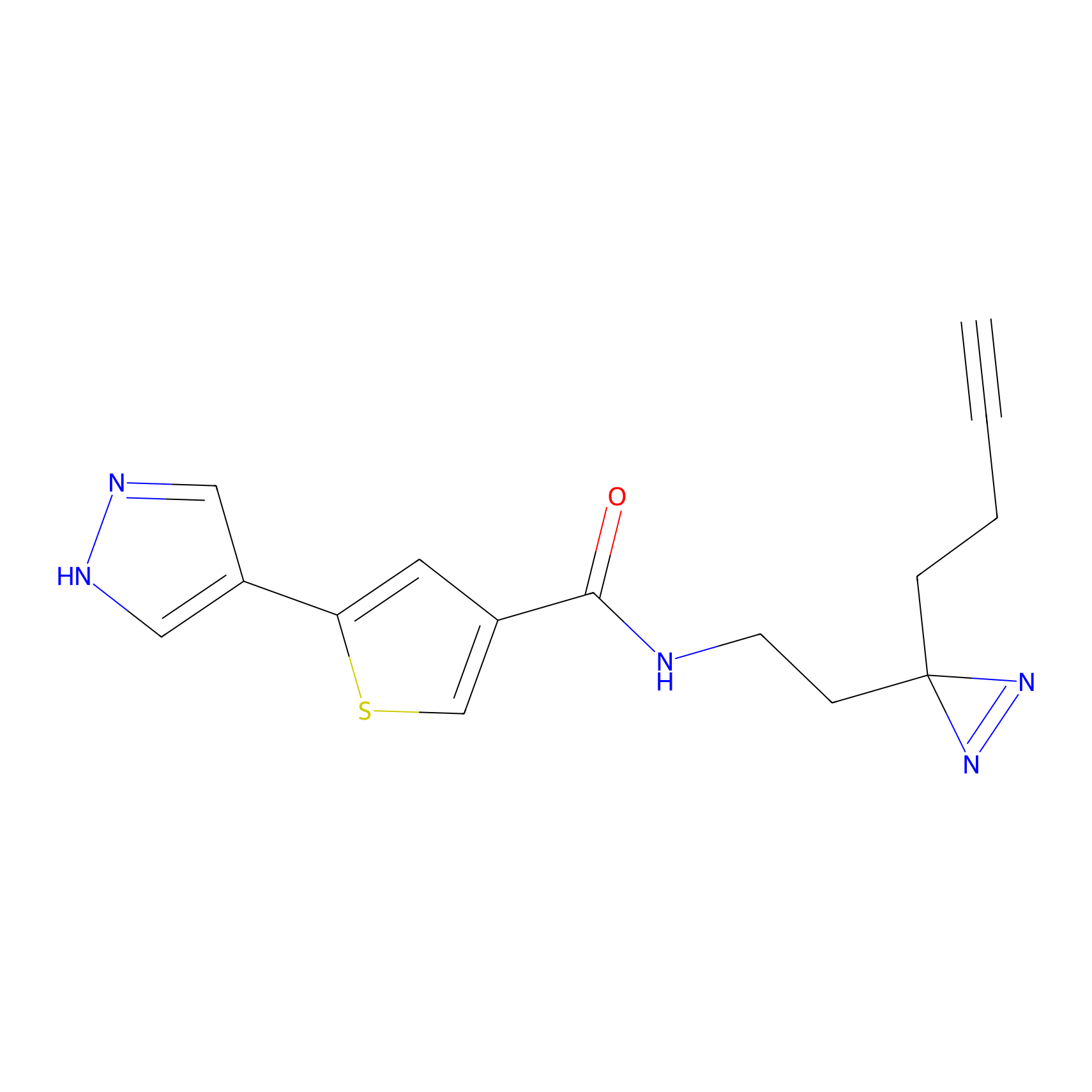
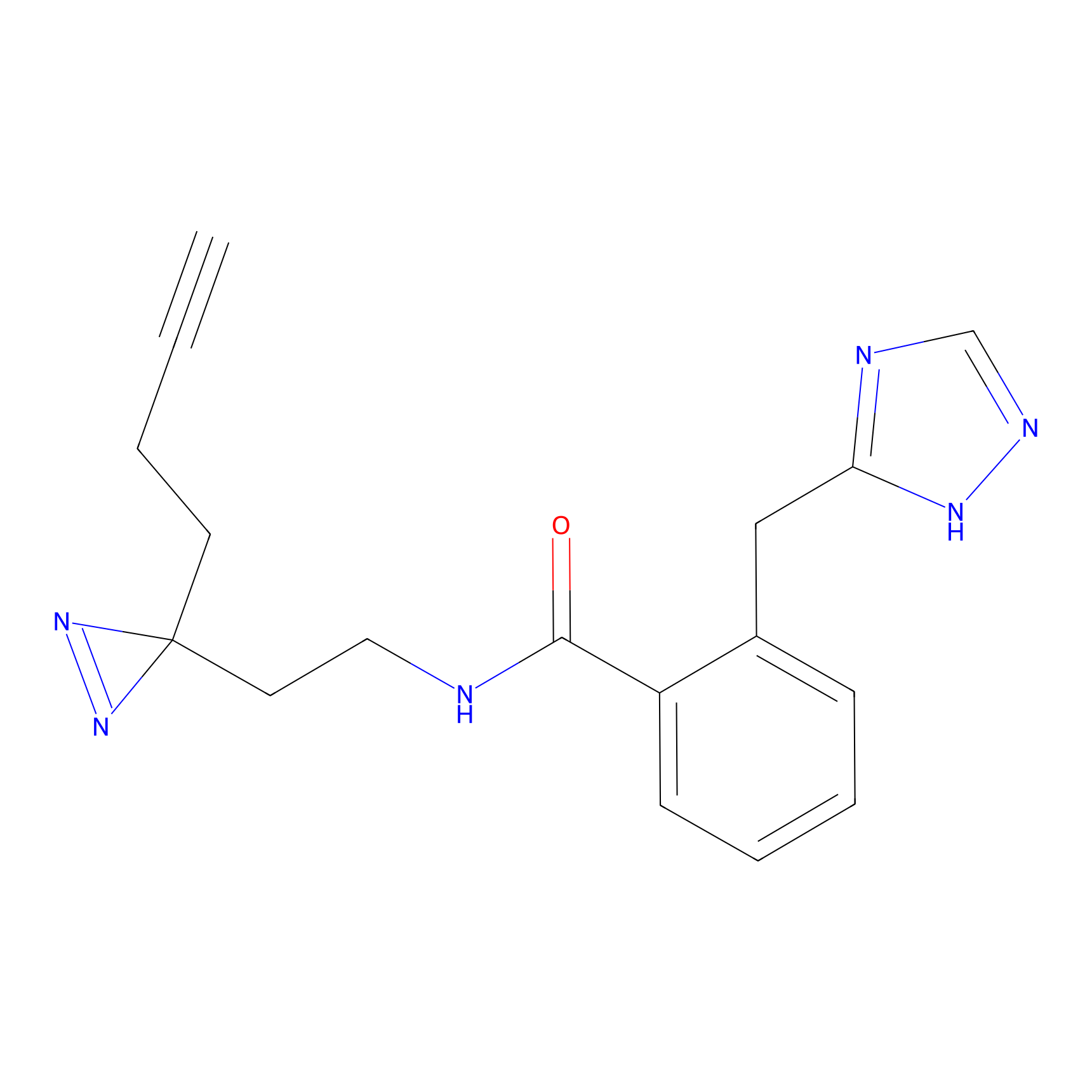
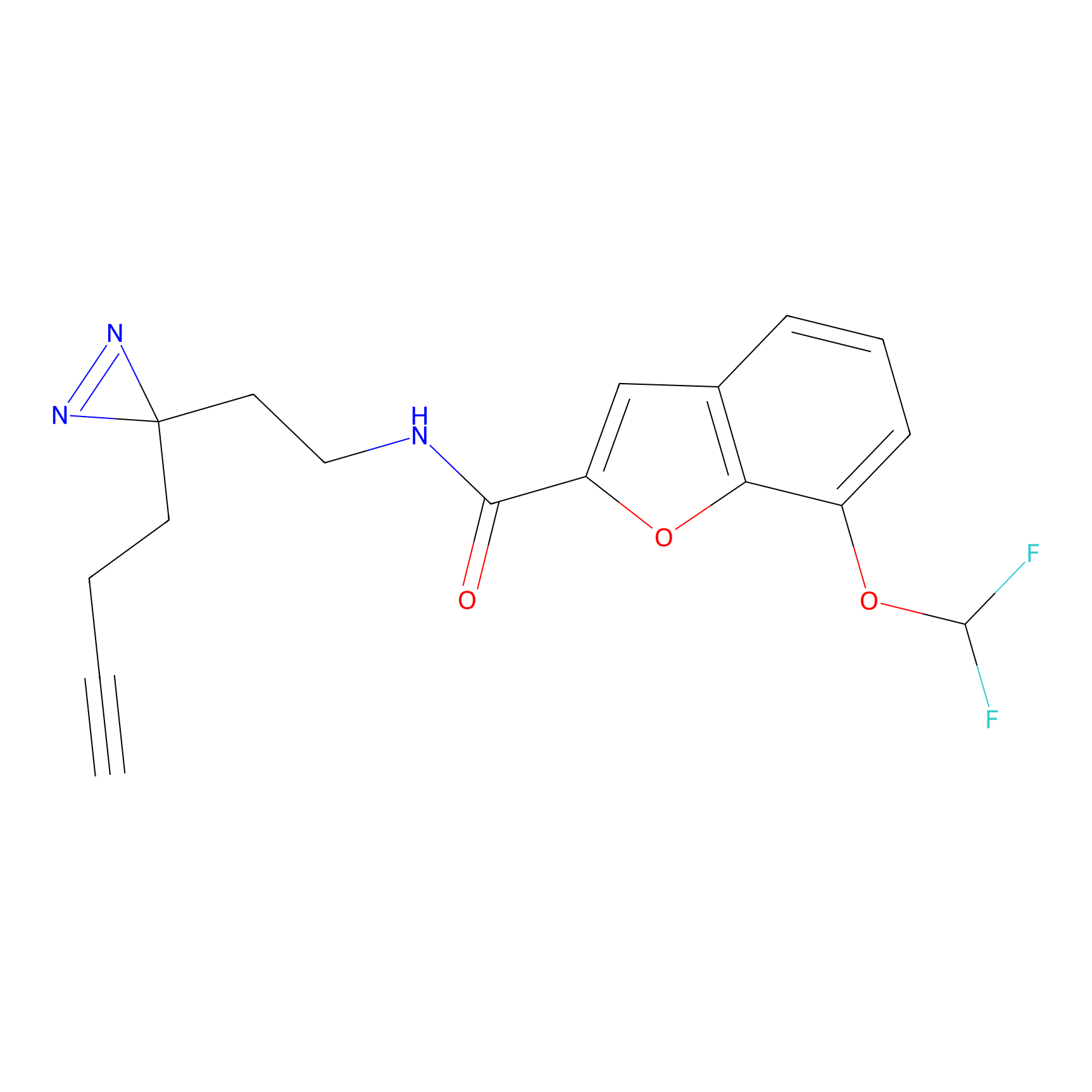
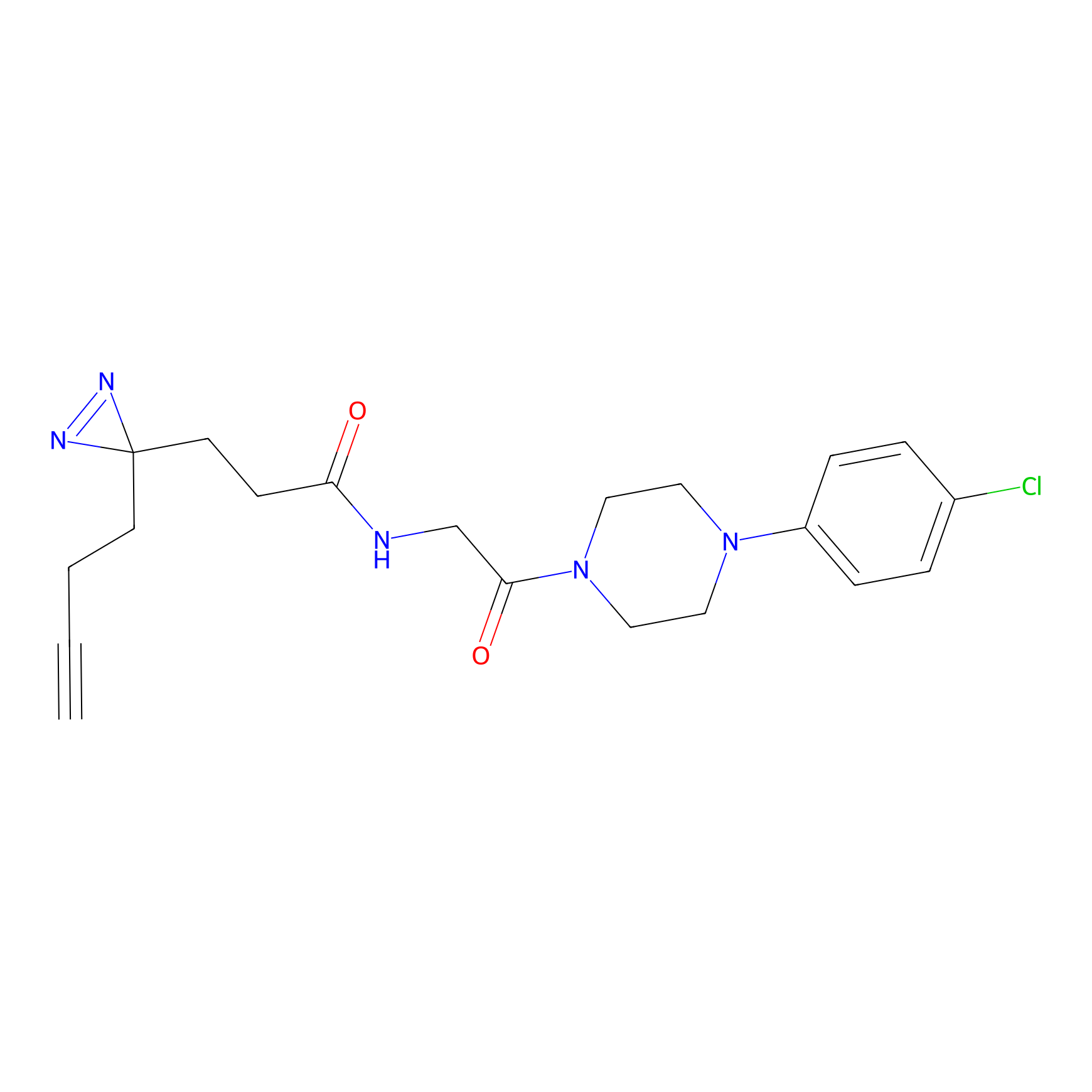
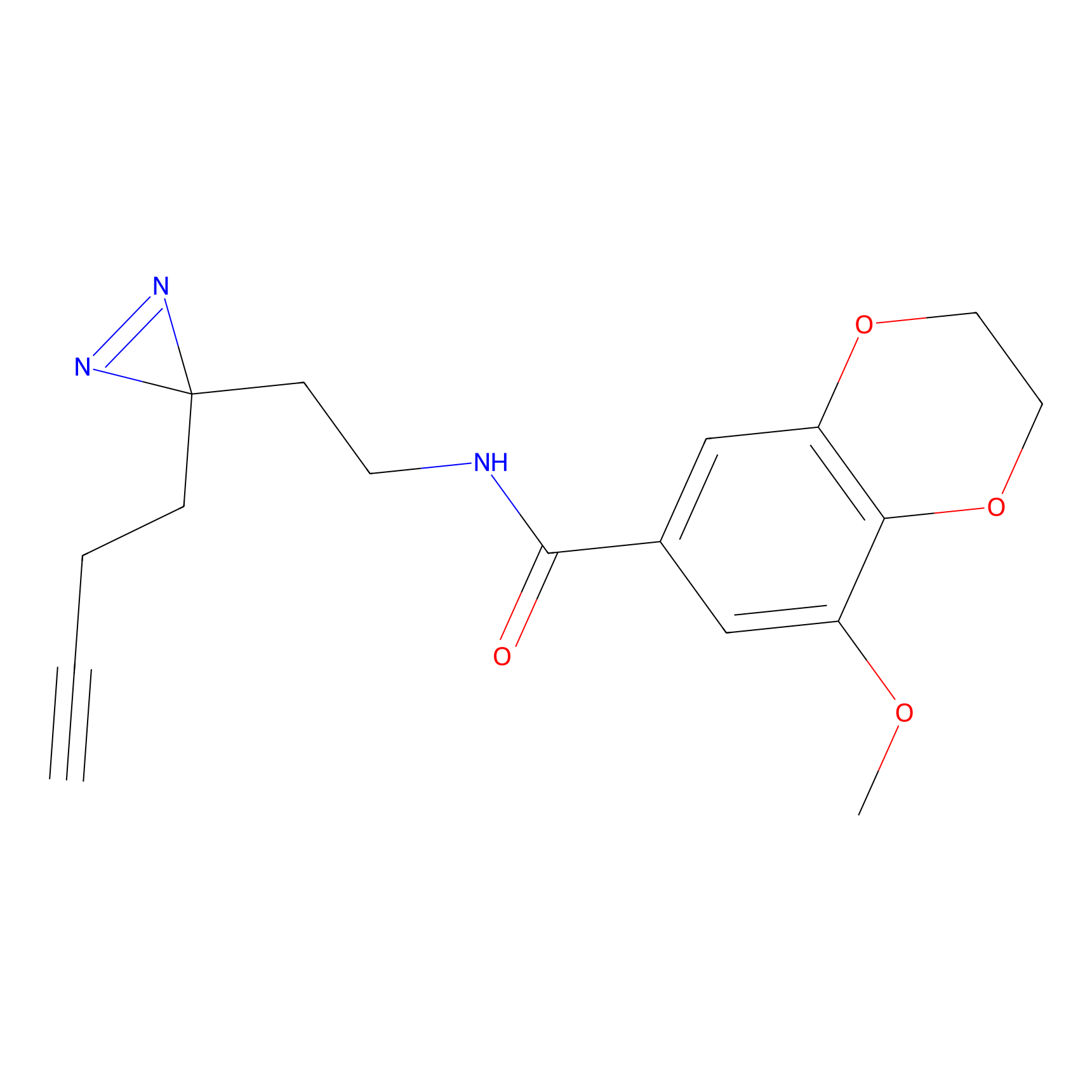
STPyne Probe Info |
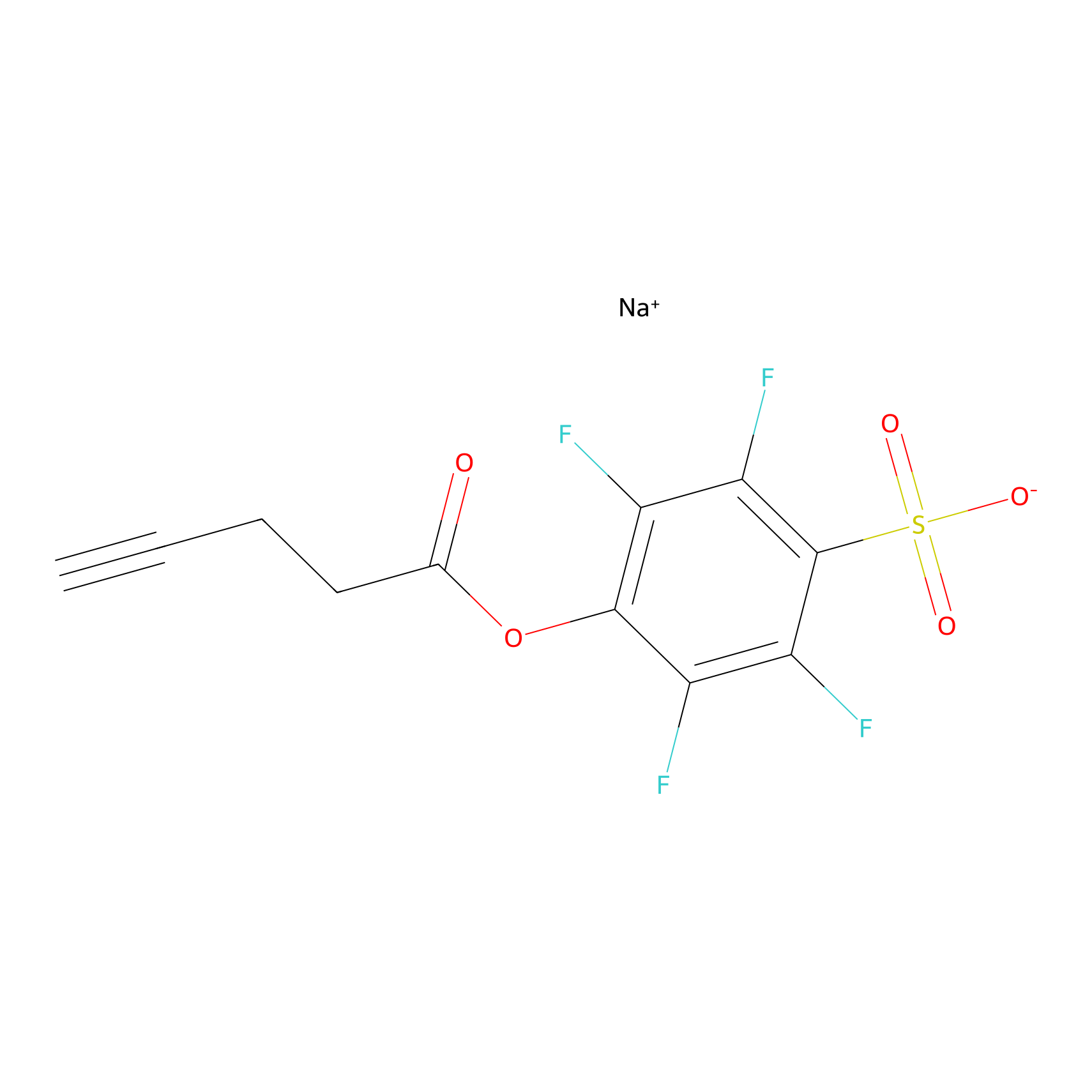 |
K56(1.82) | LDD0277 | [1] | |
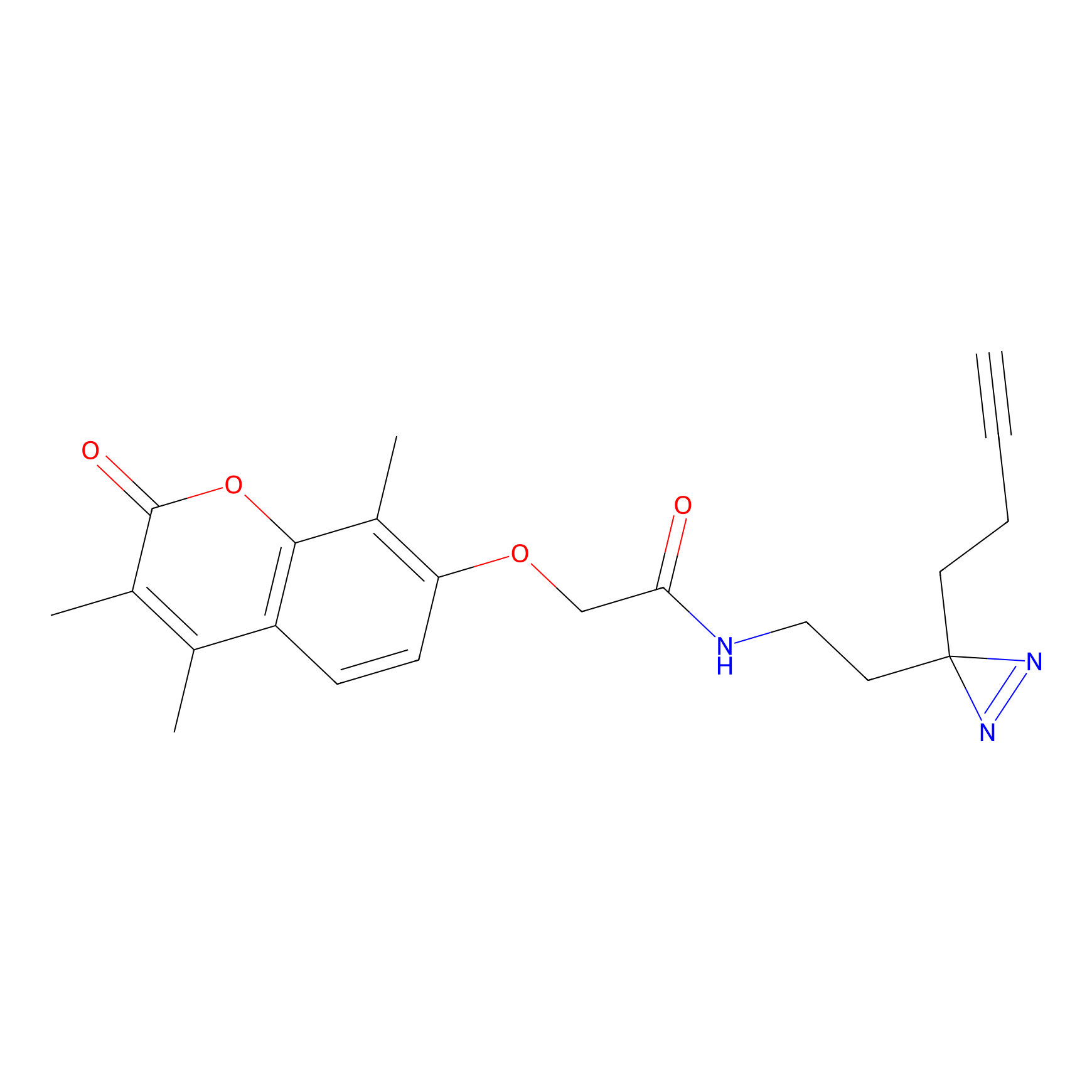
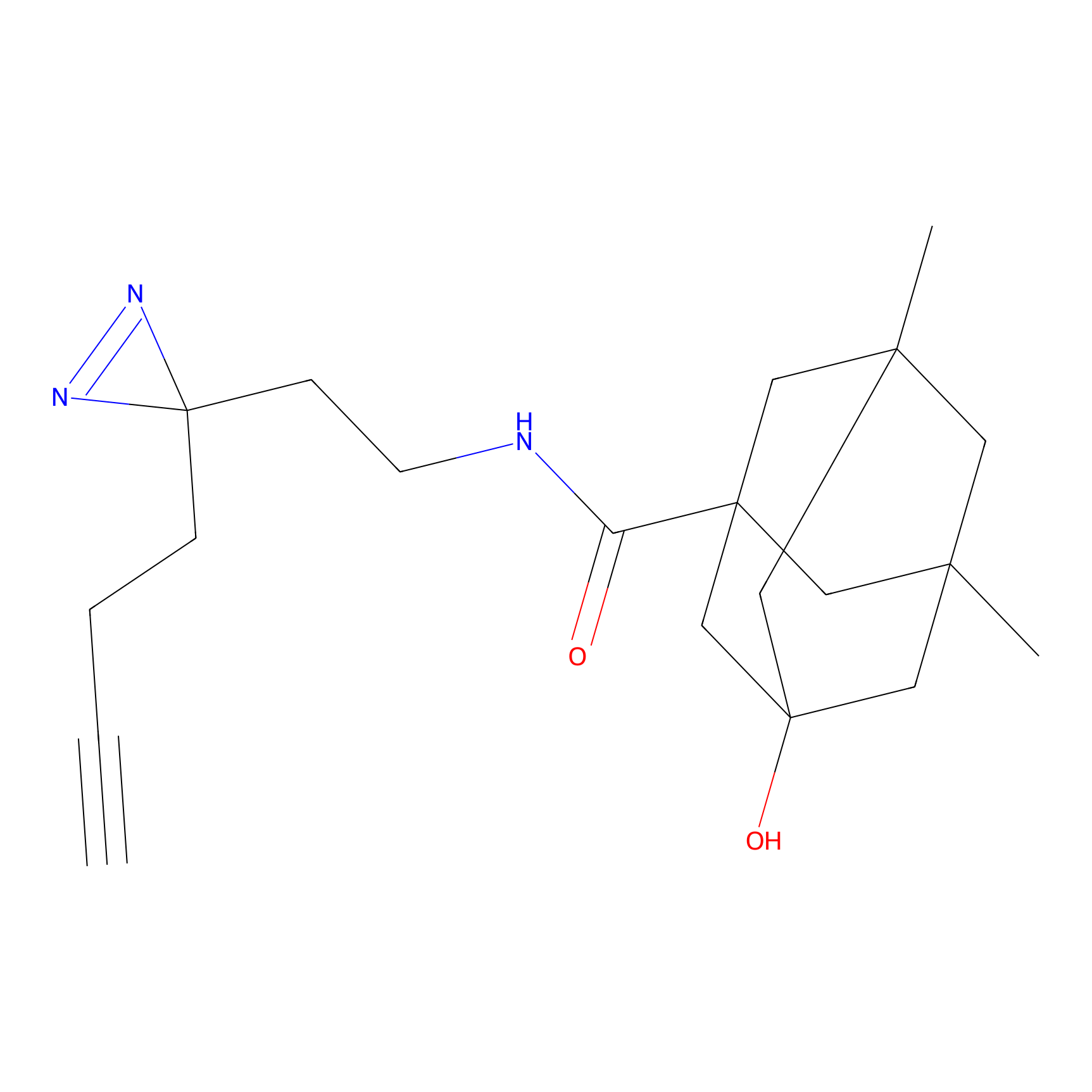
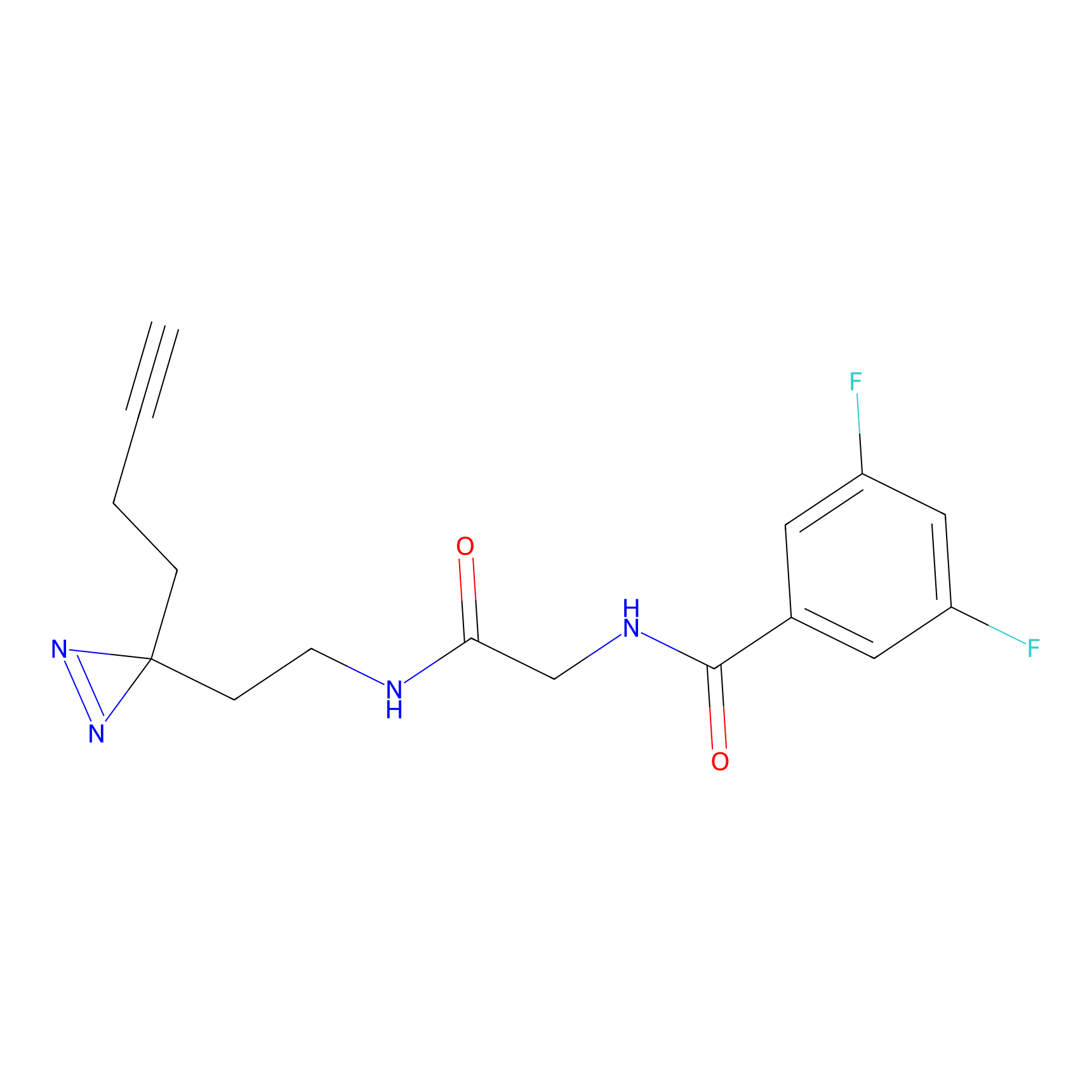
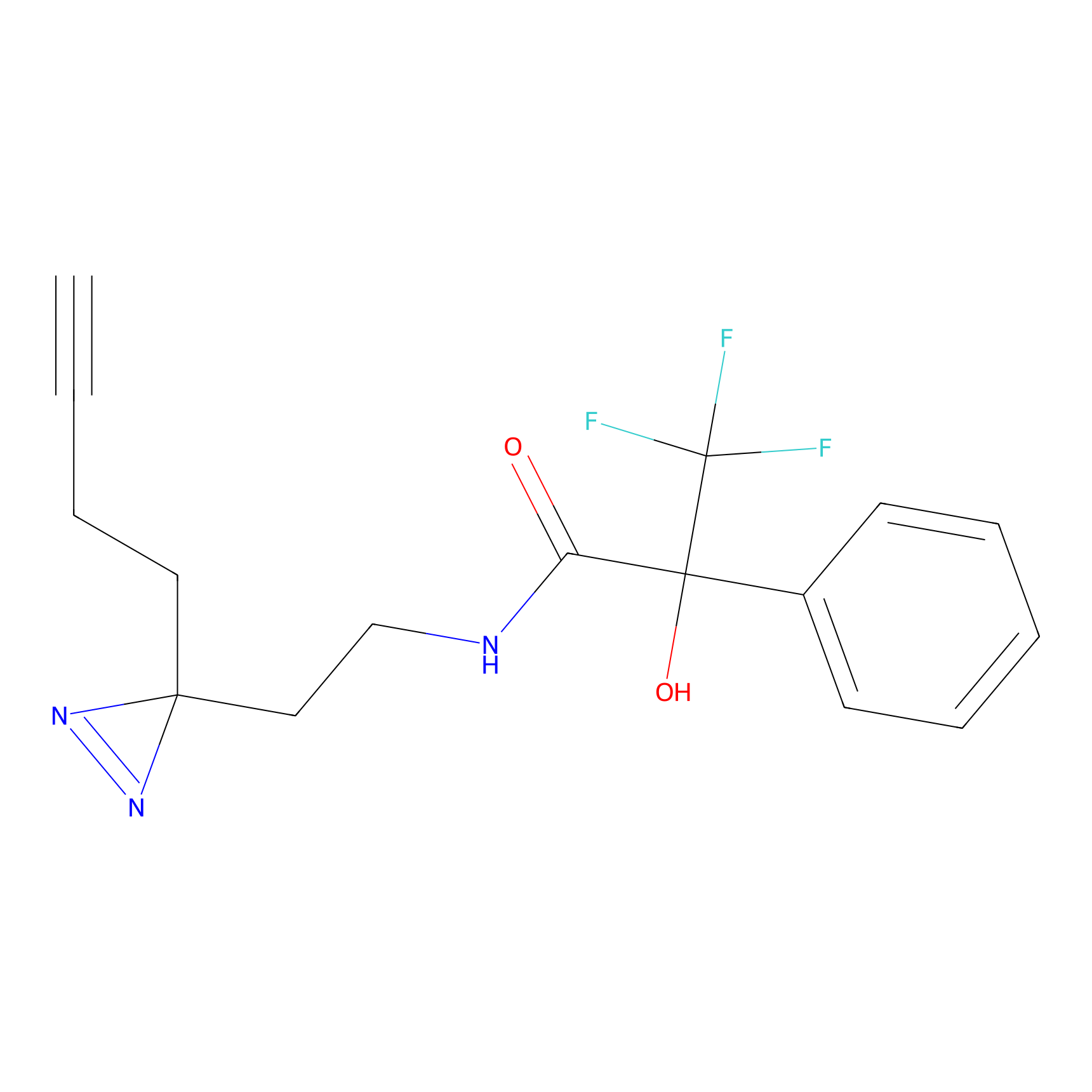
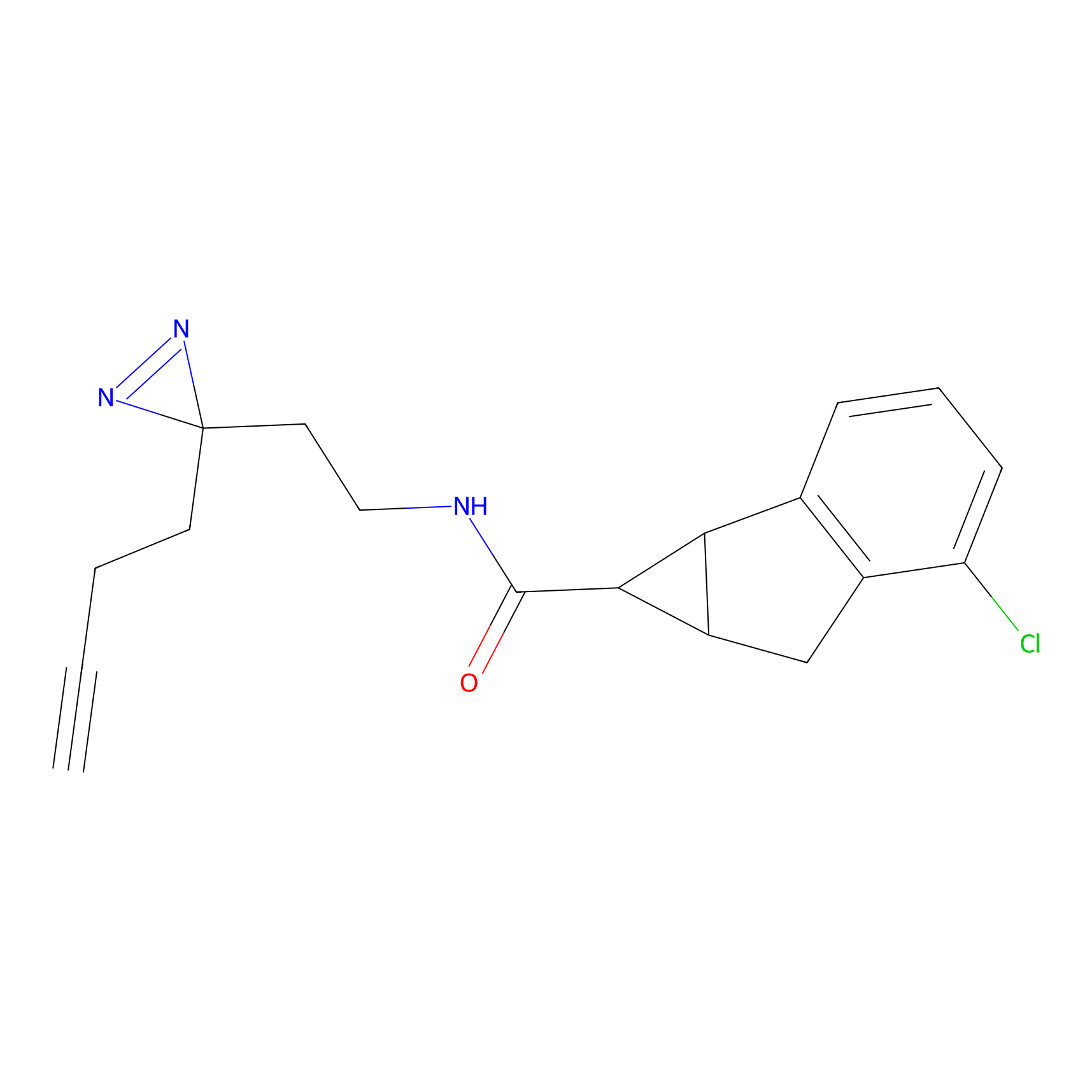
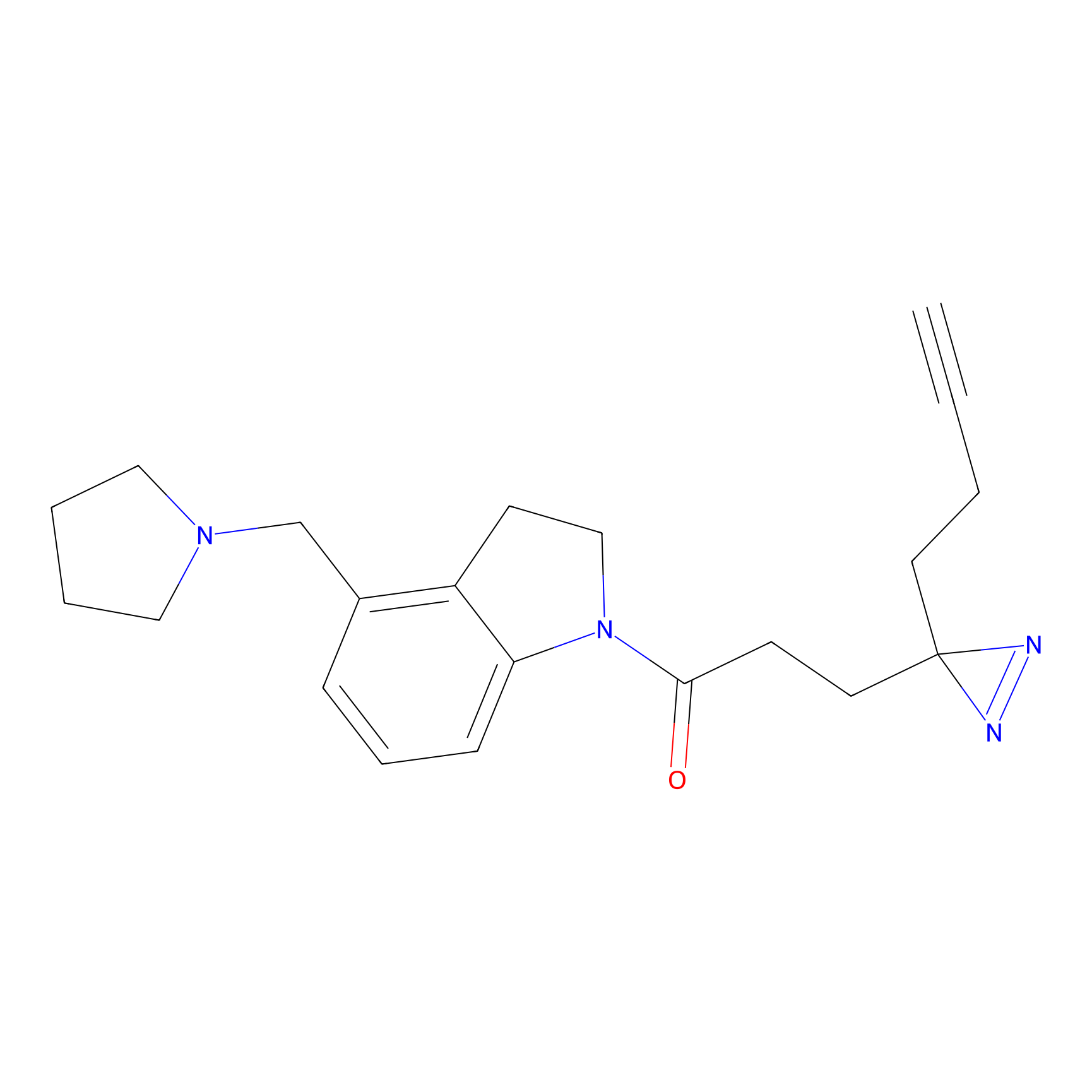
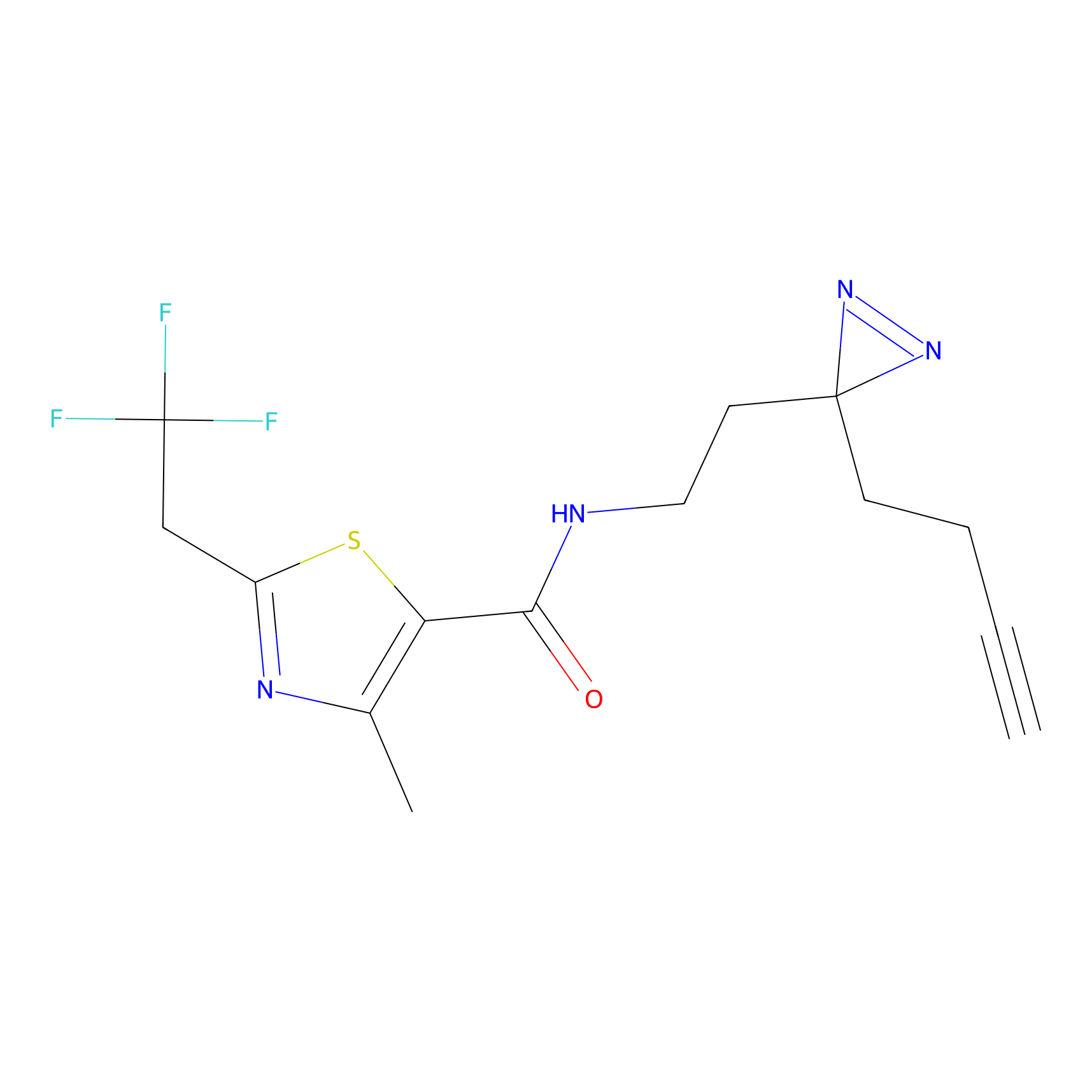
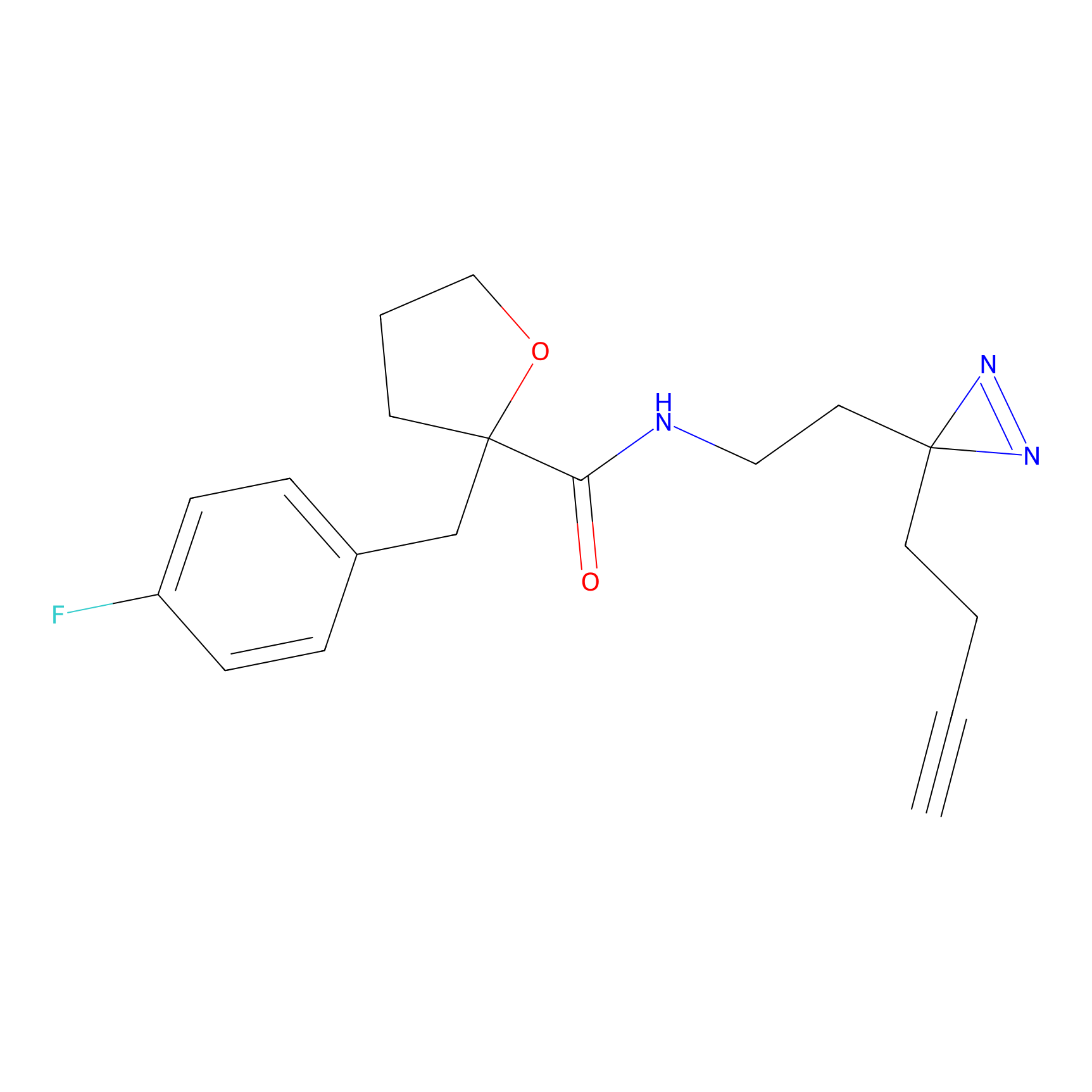
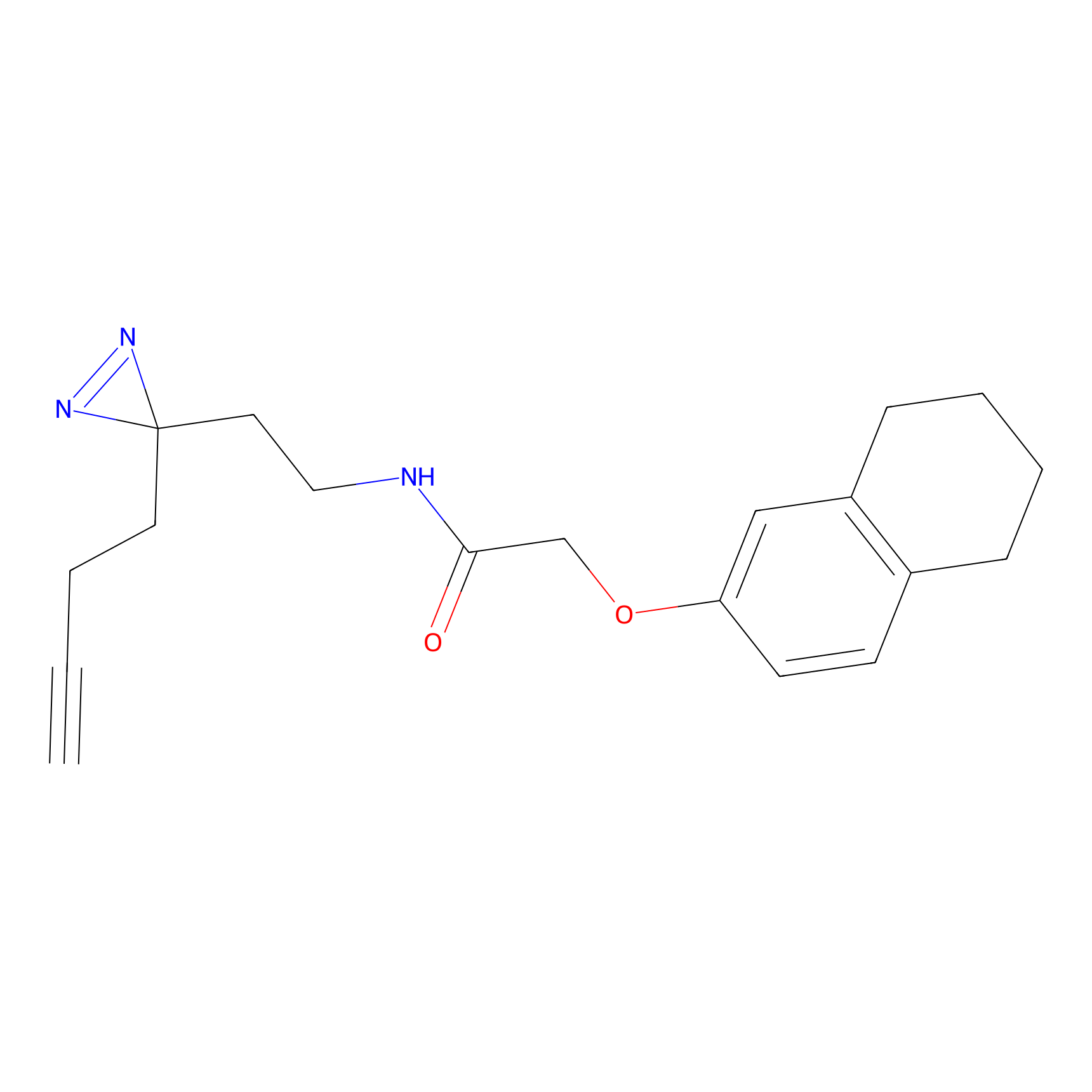
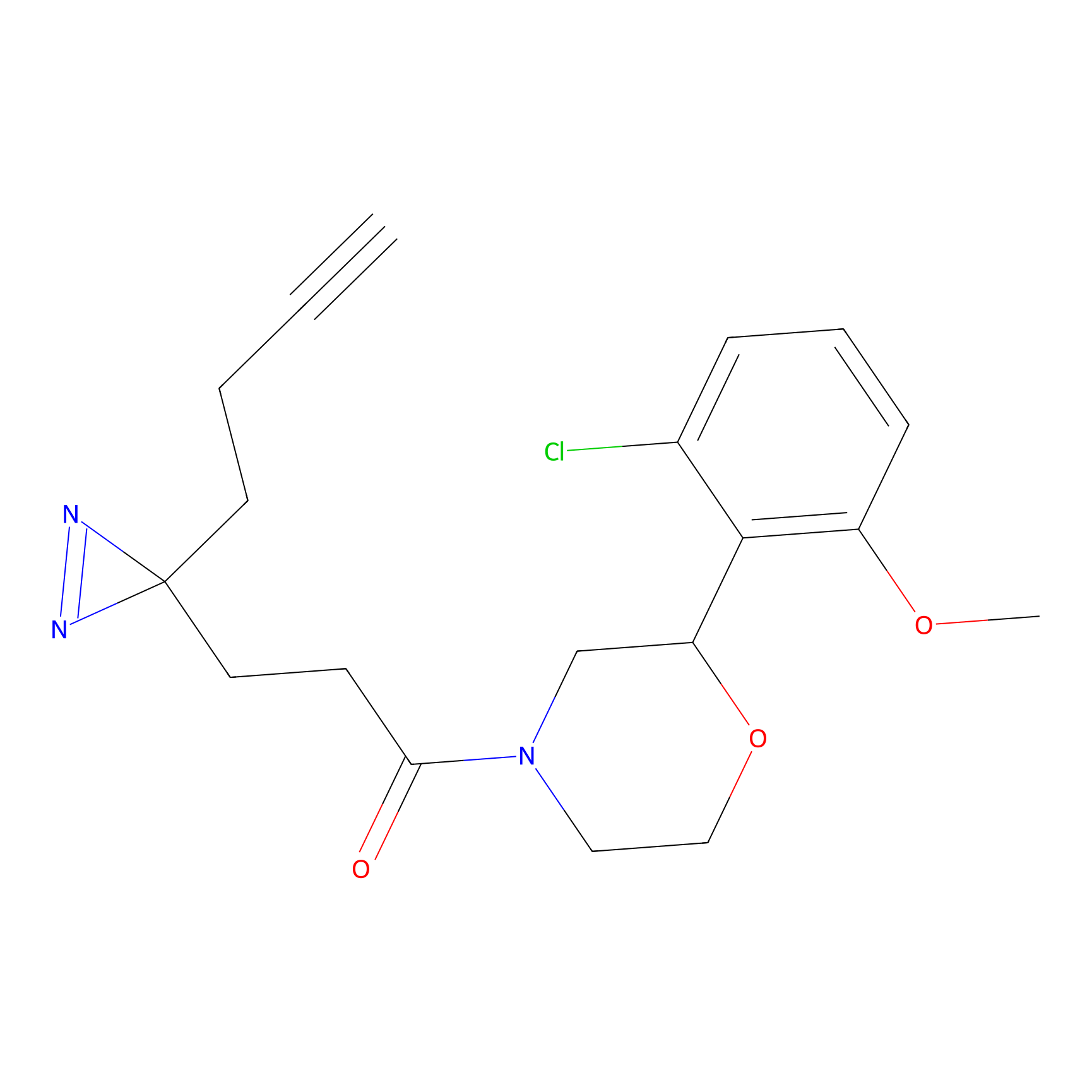
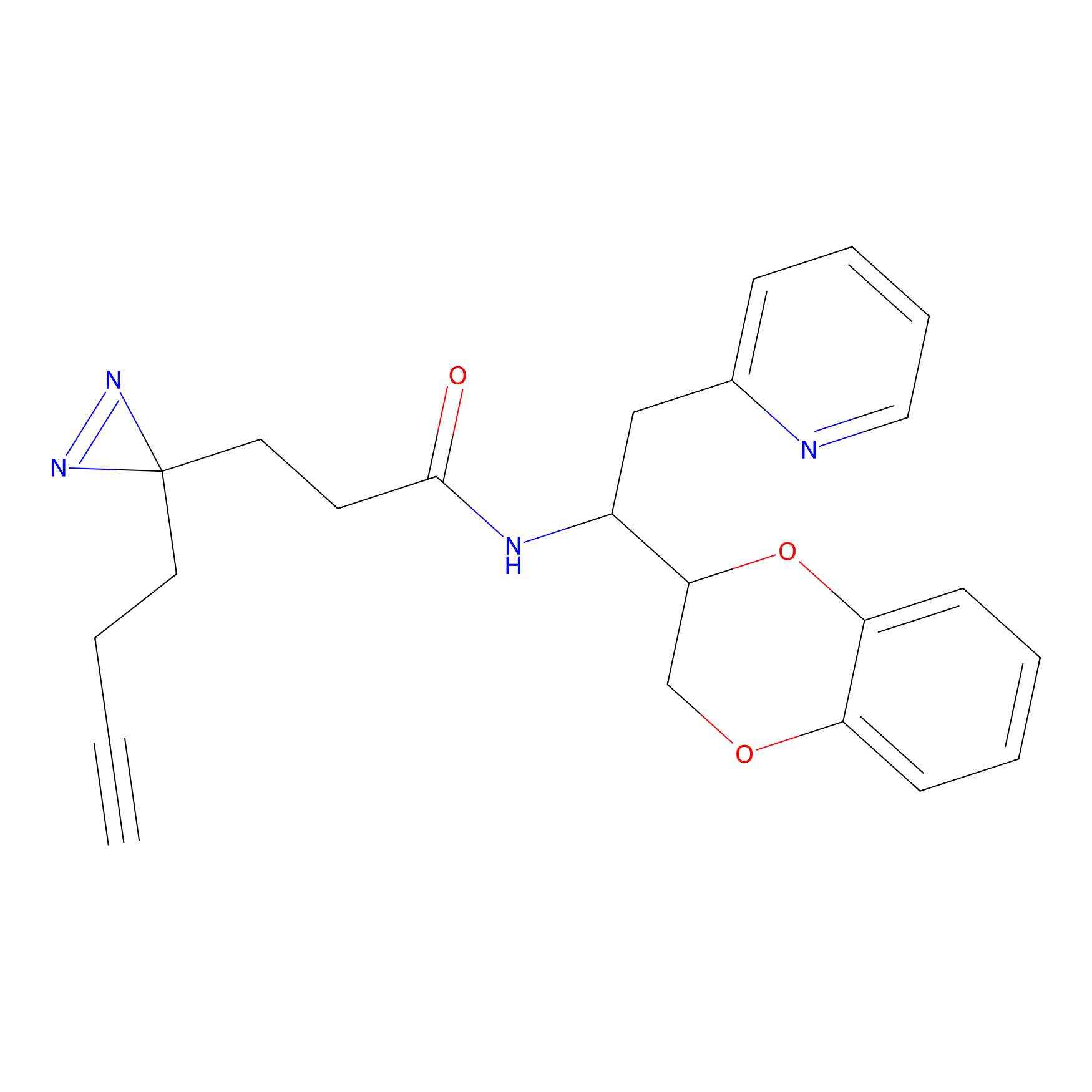
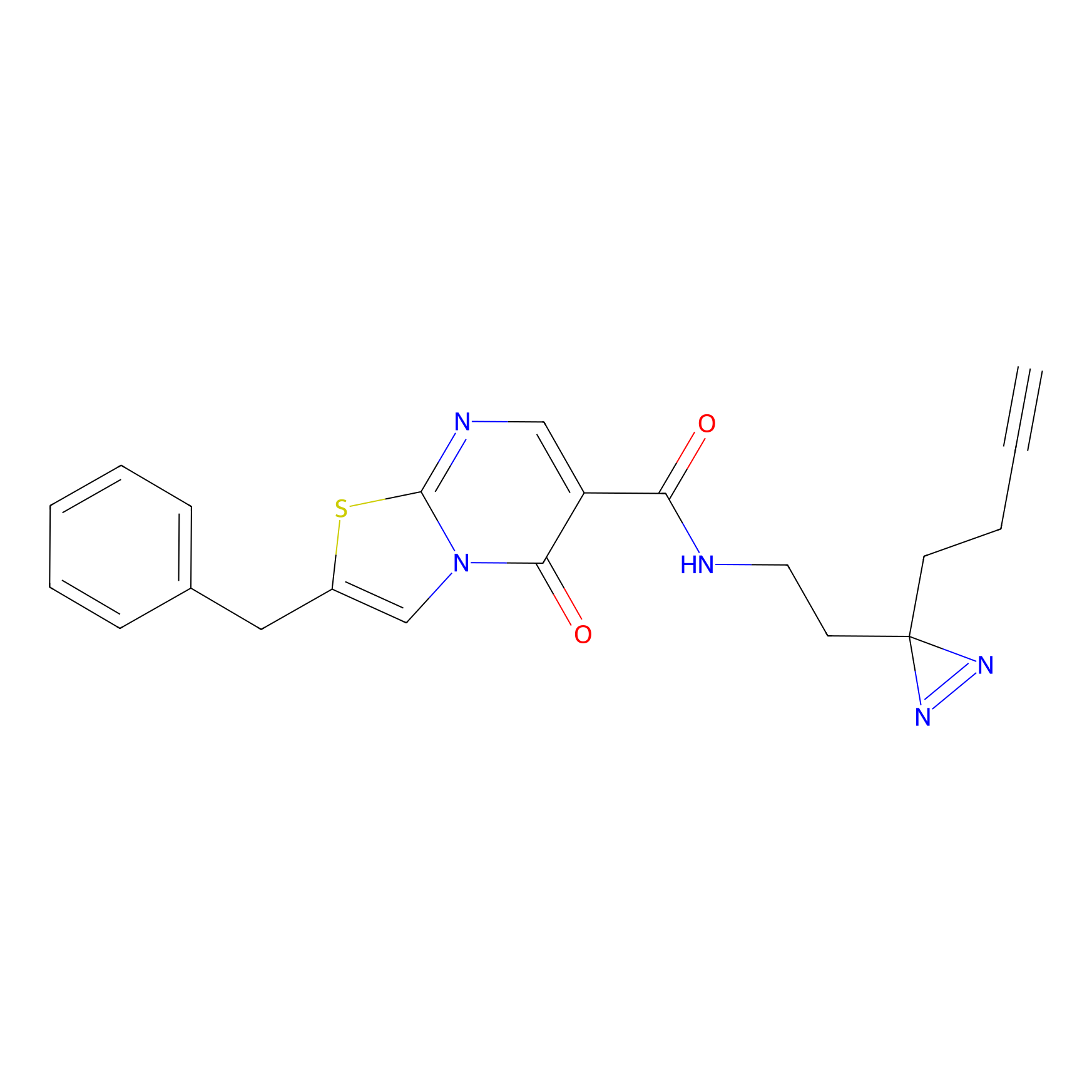
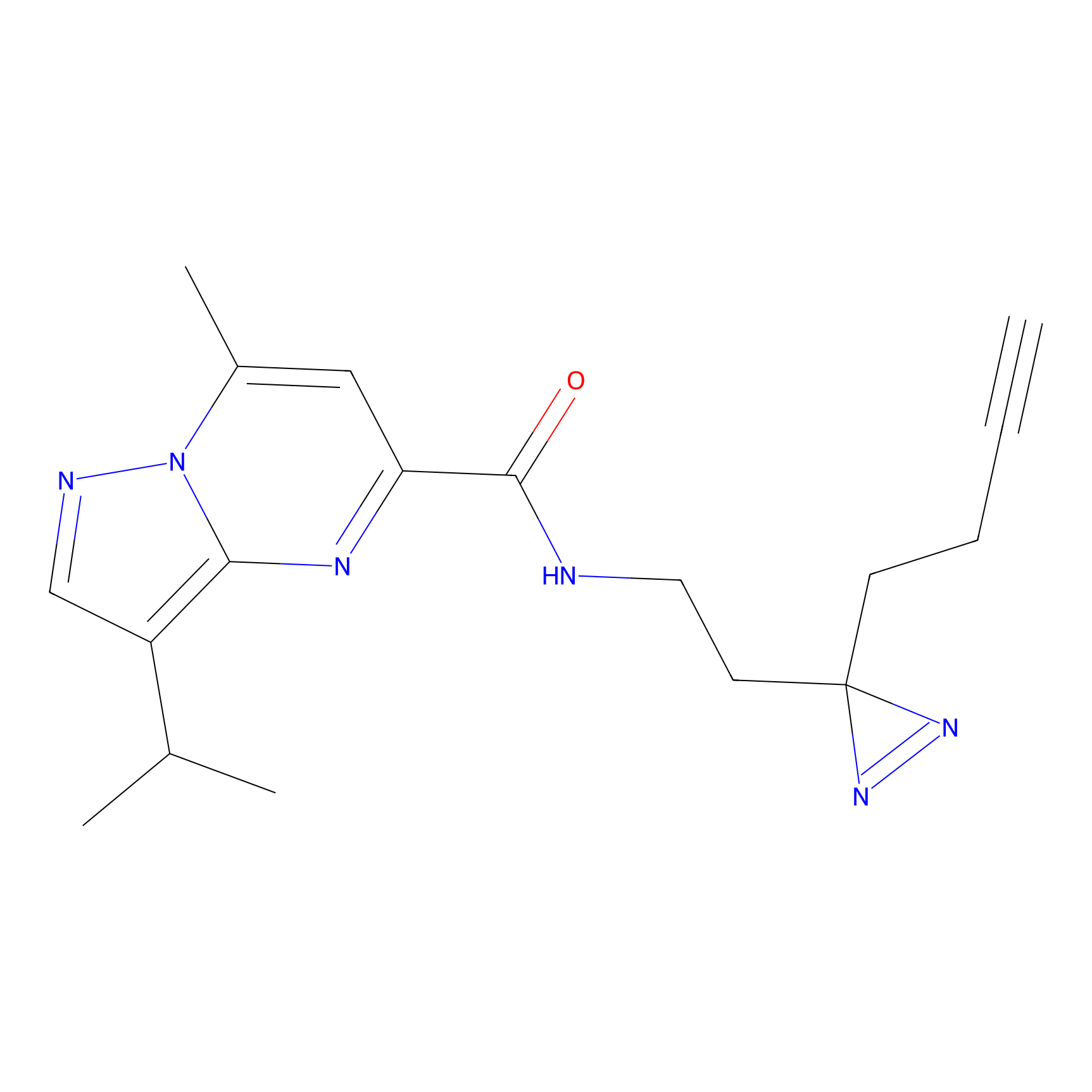
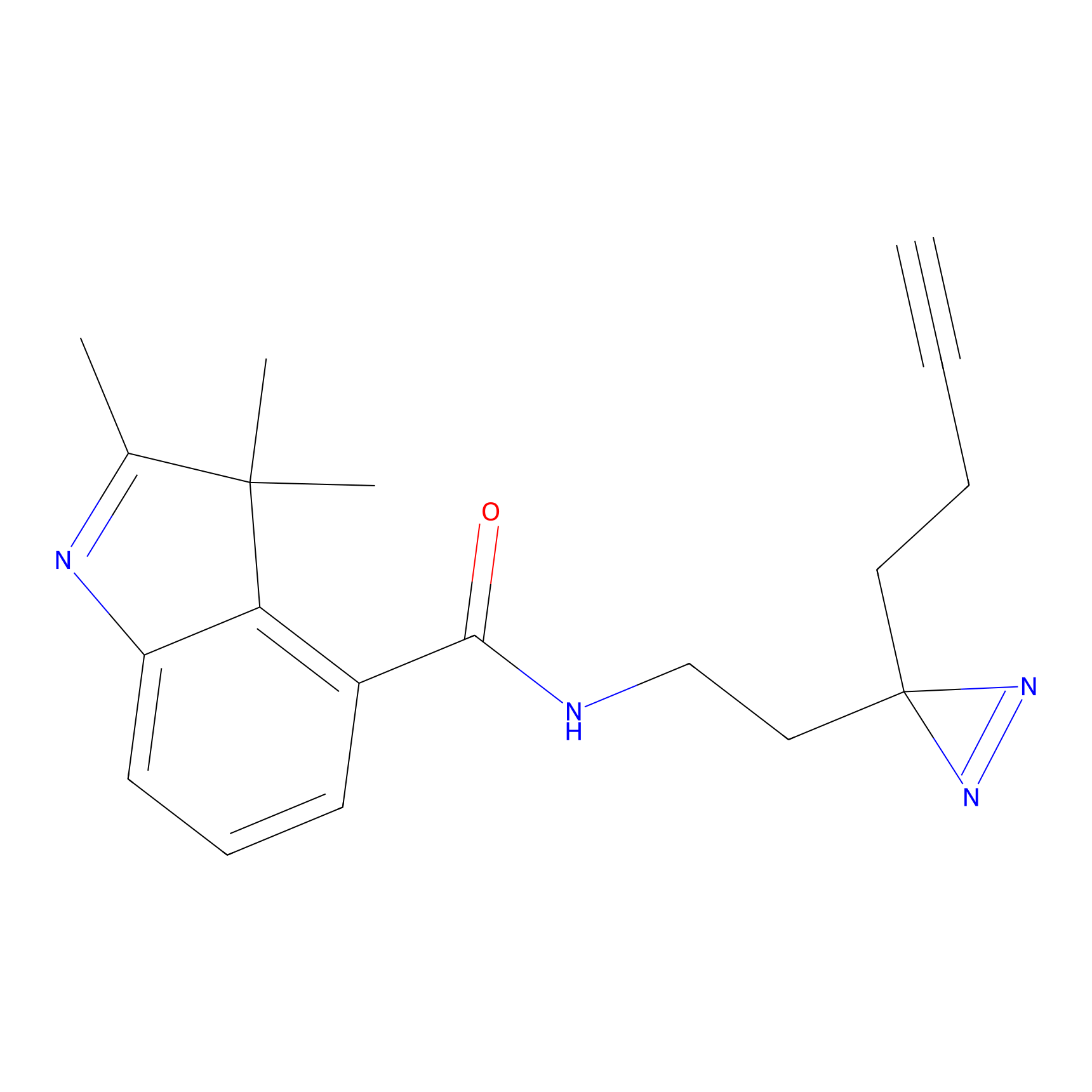
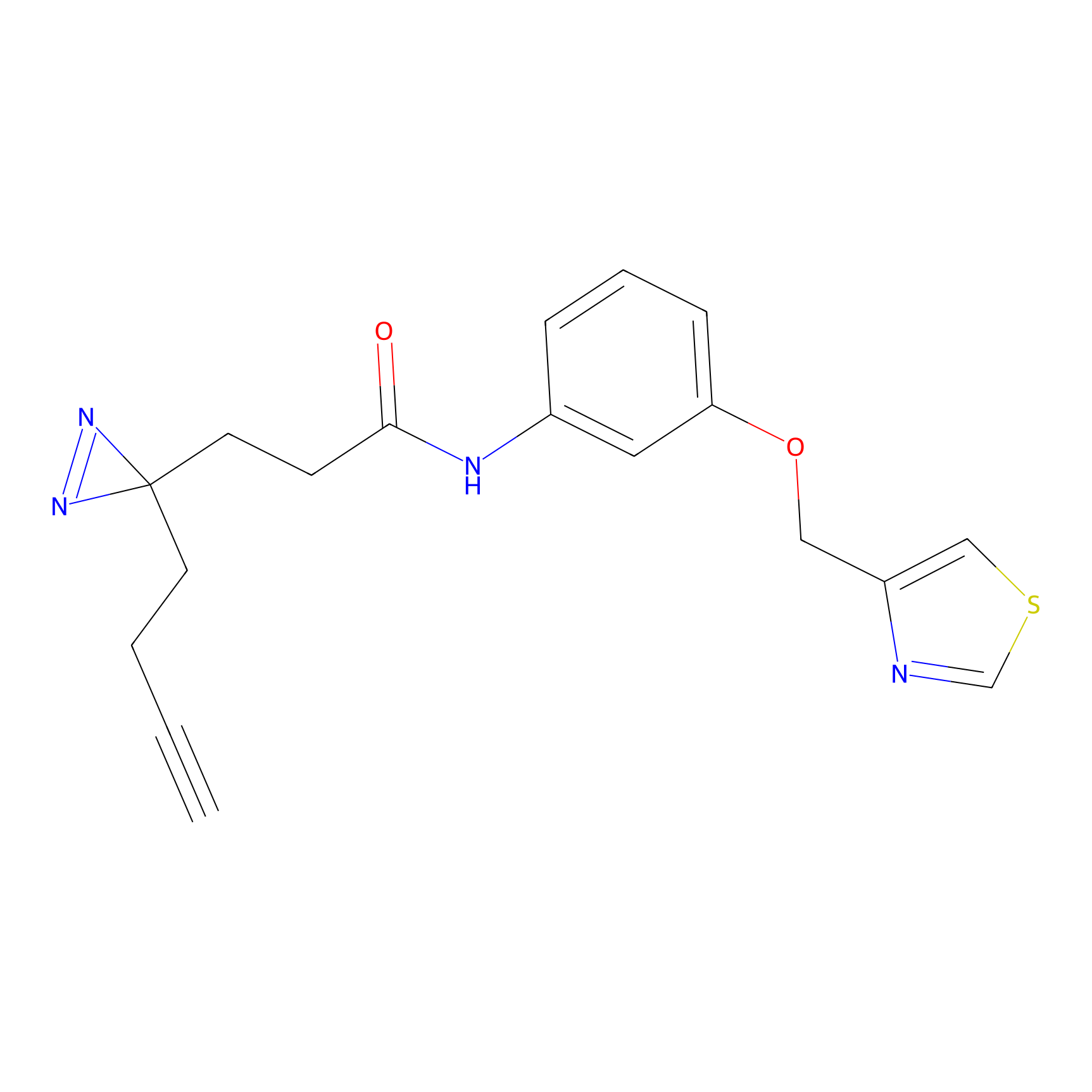
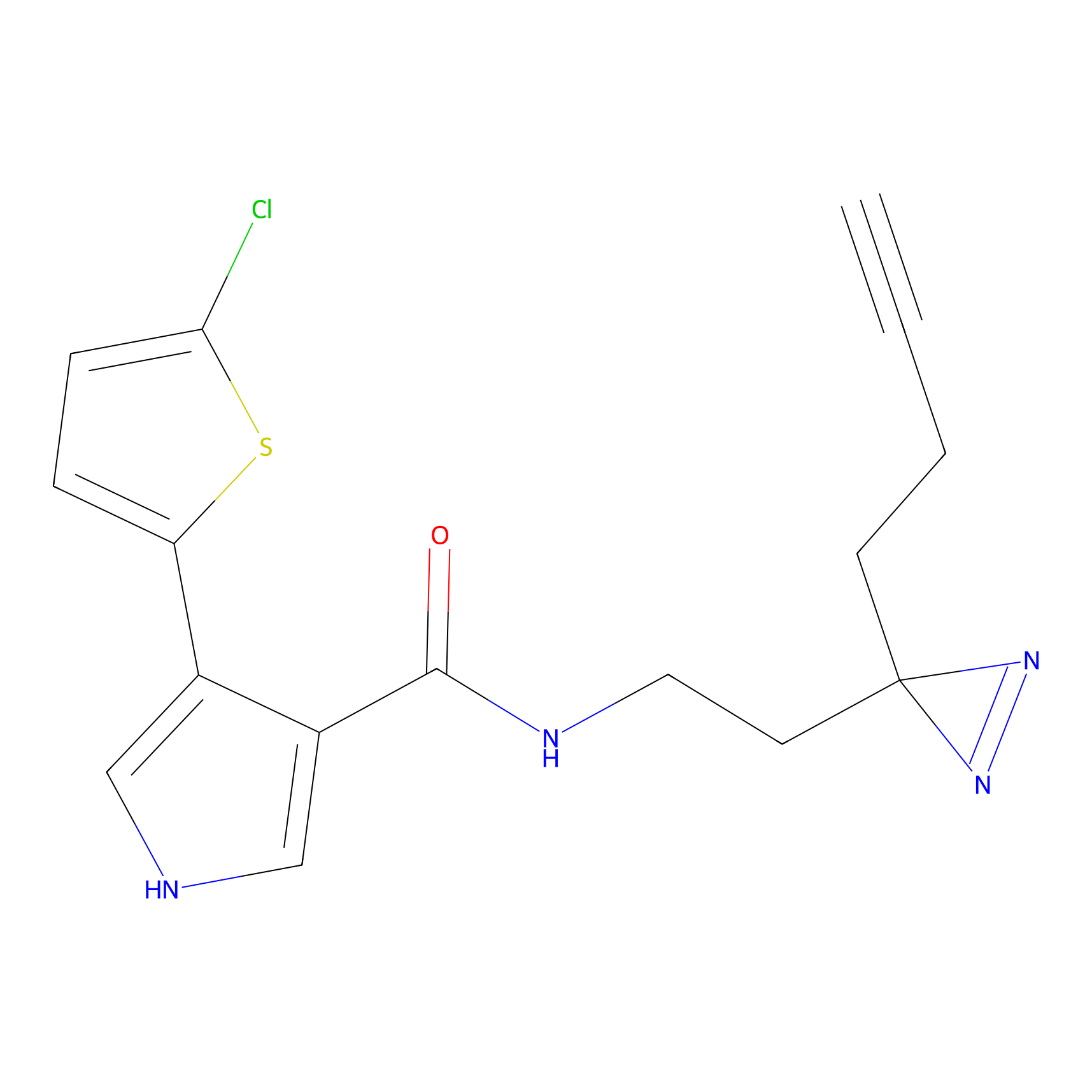
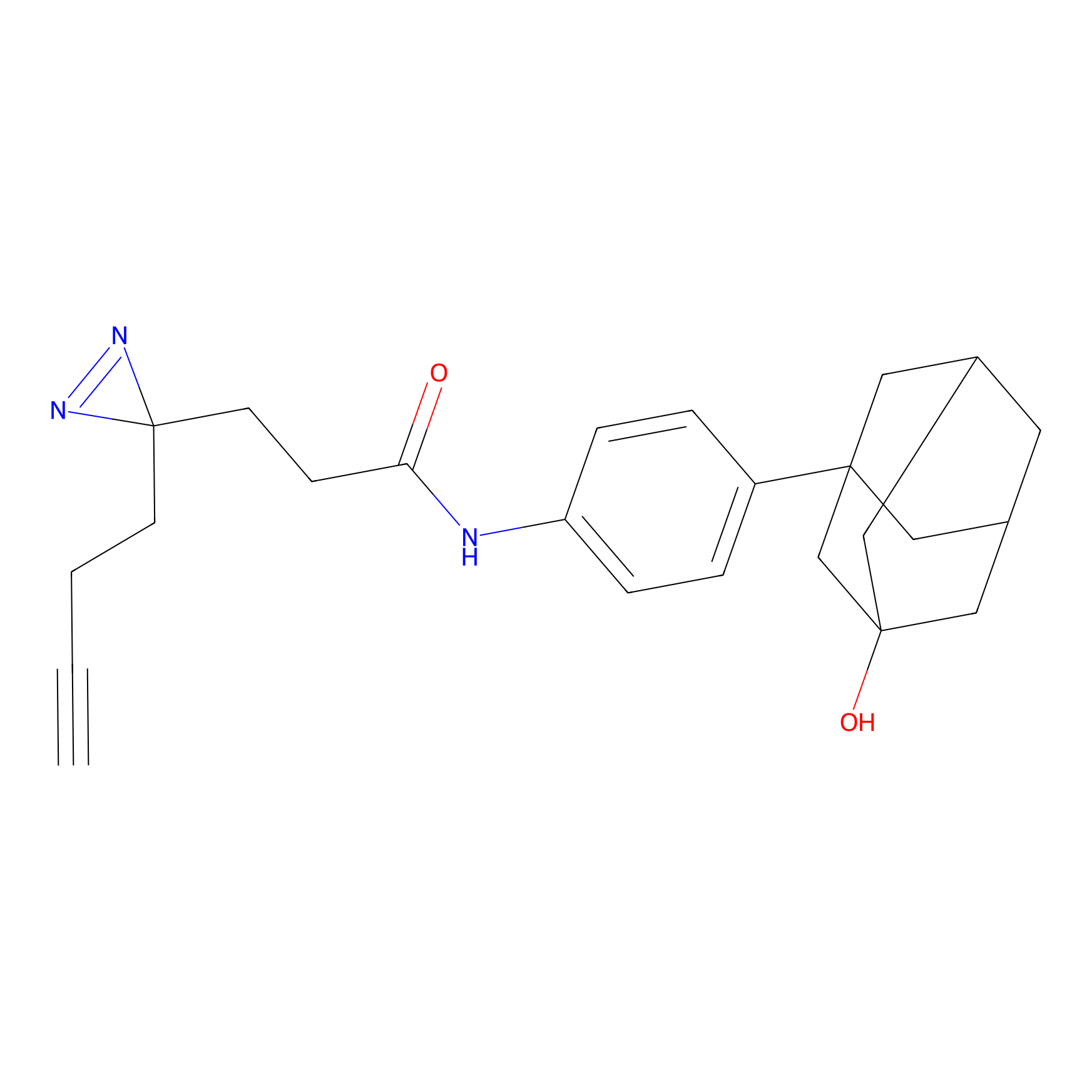
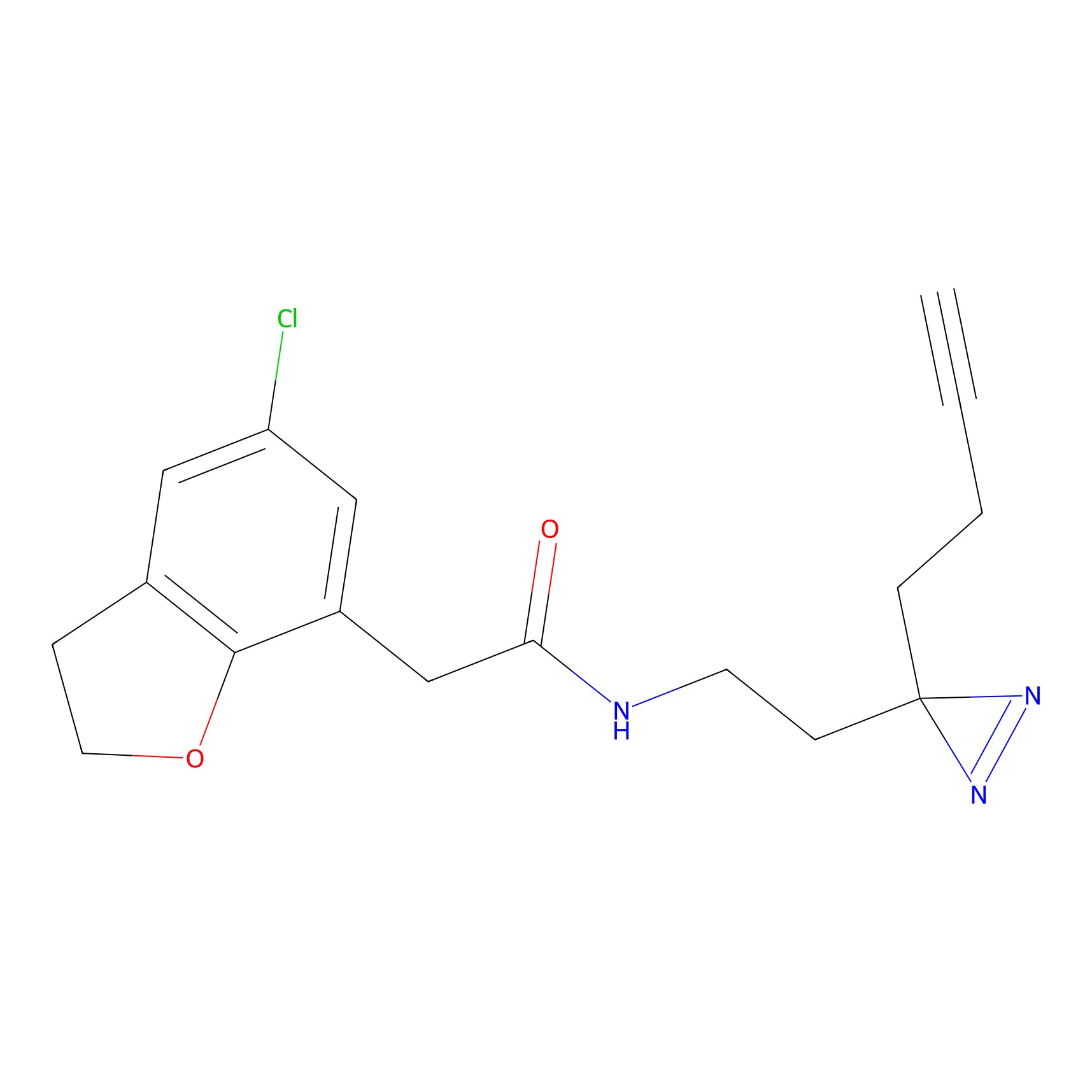
|
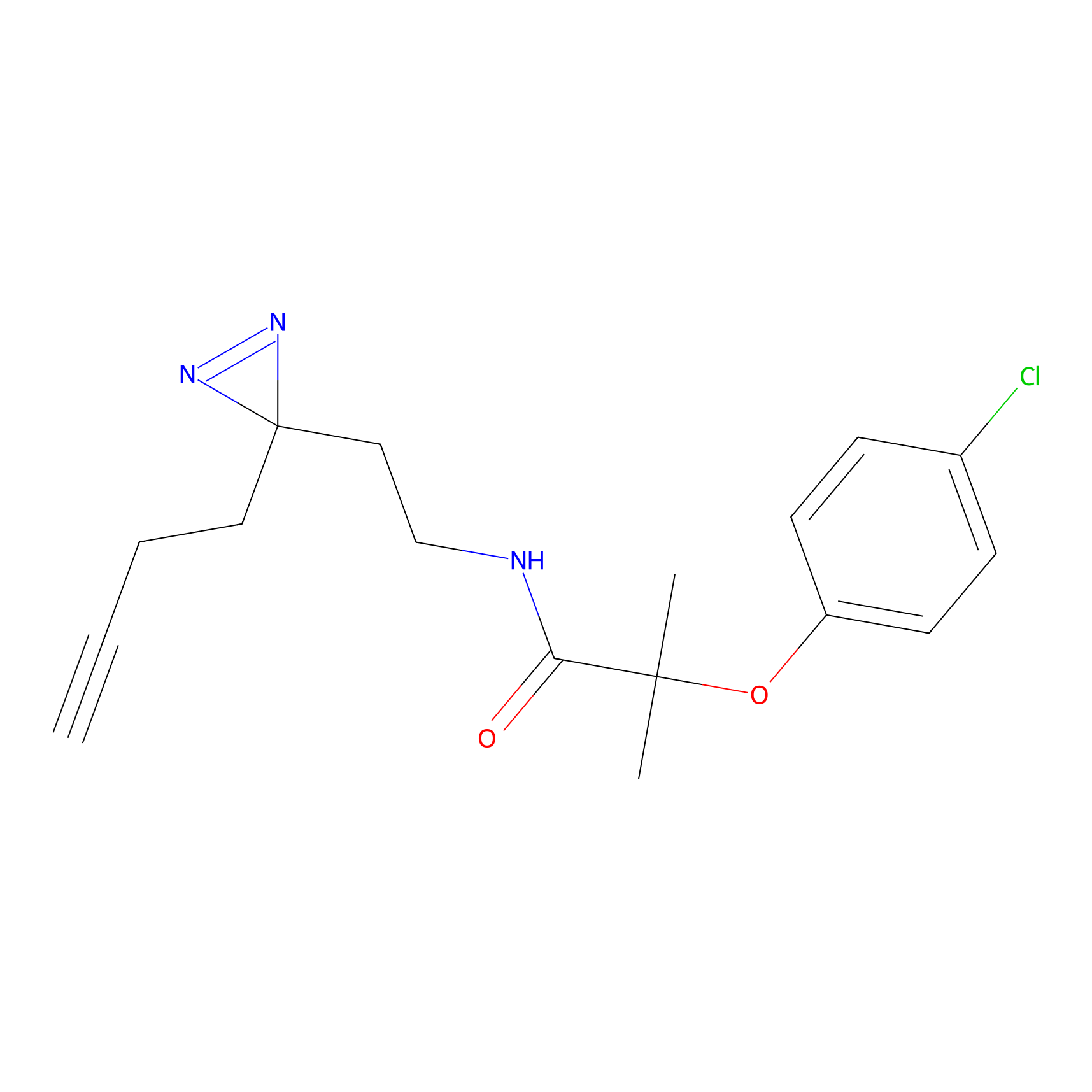
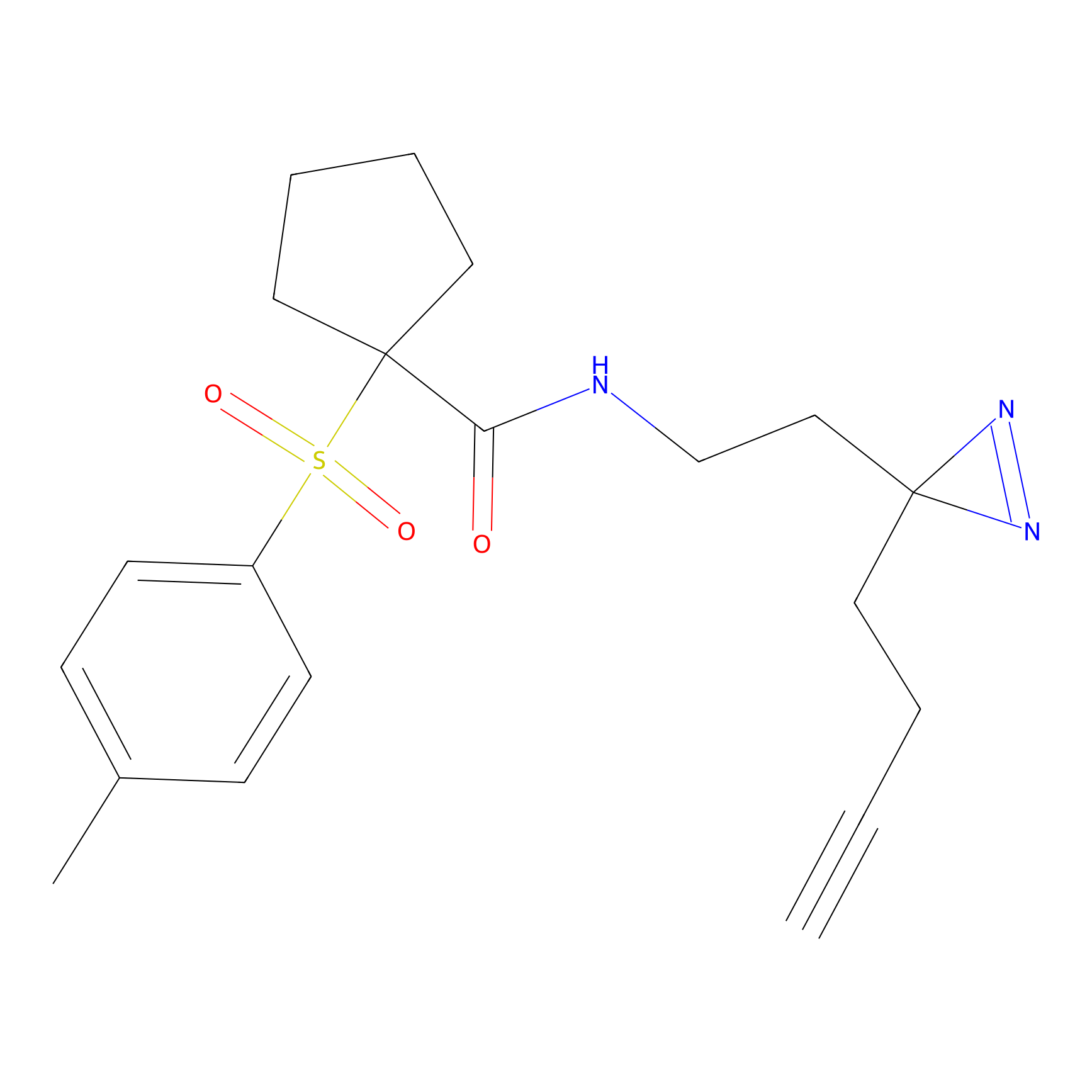
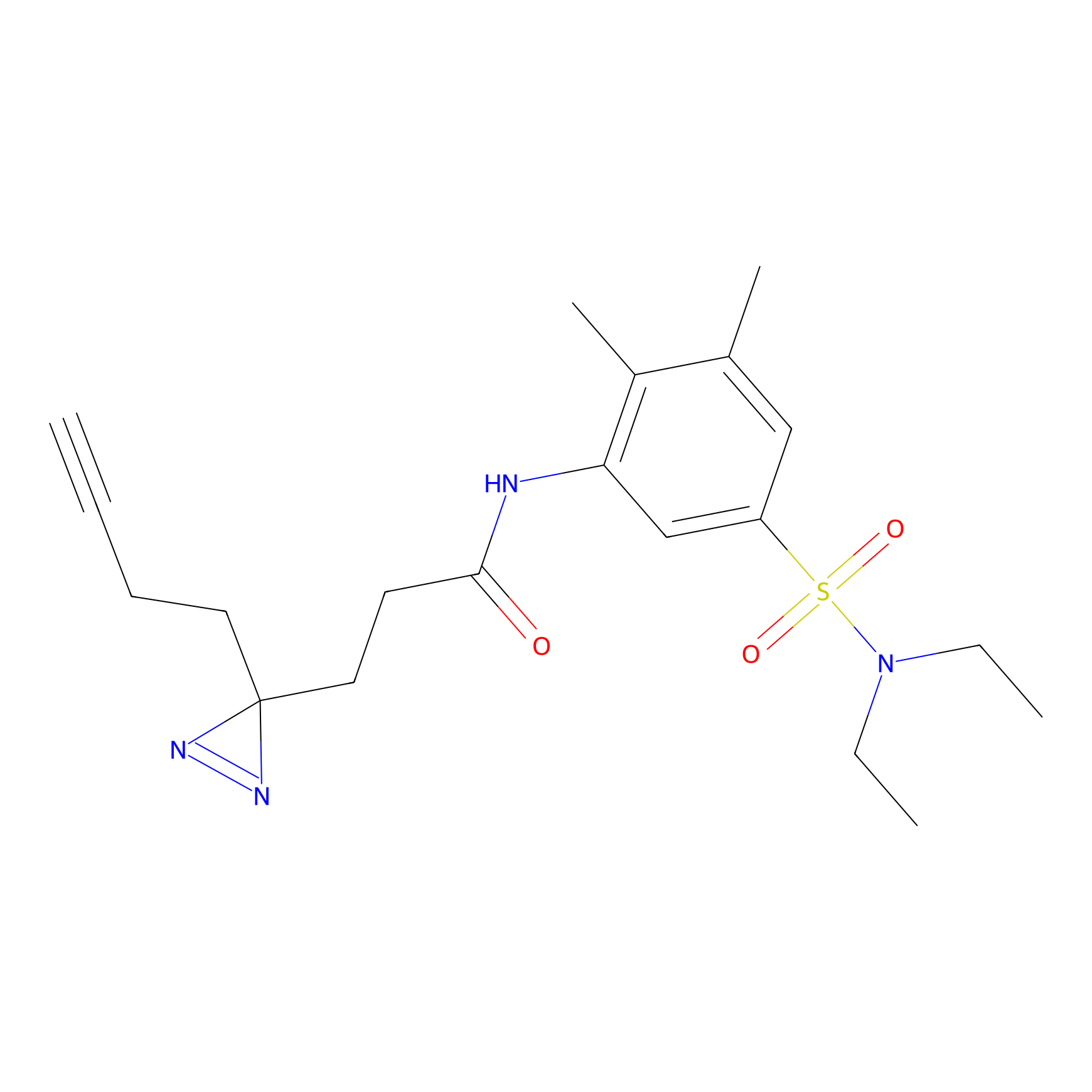
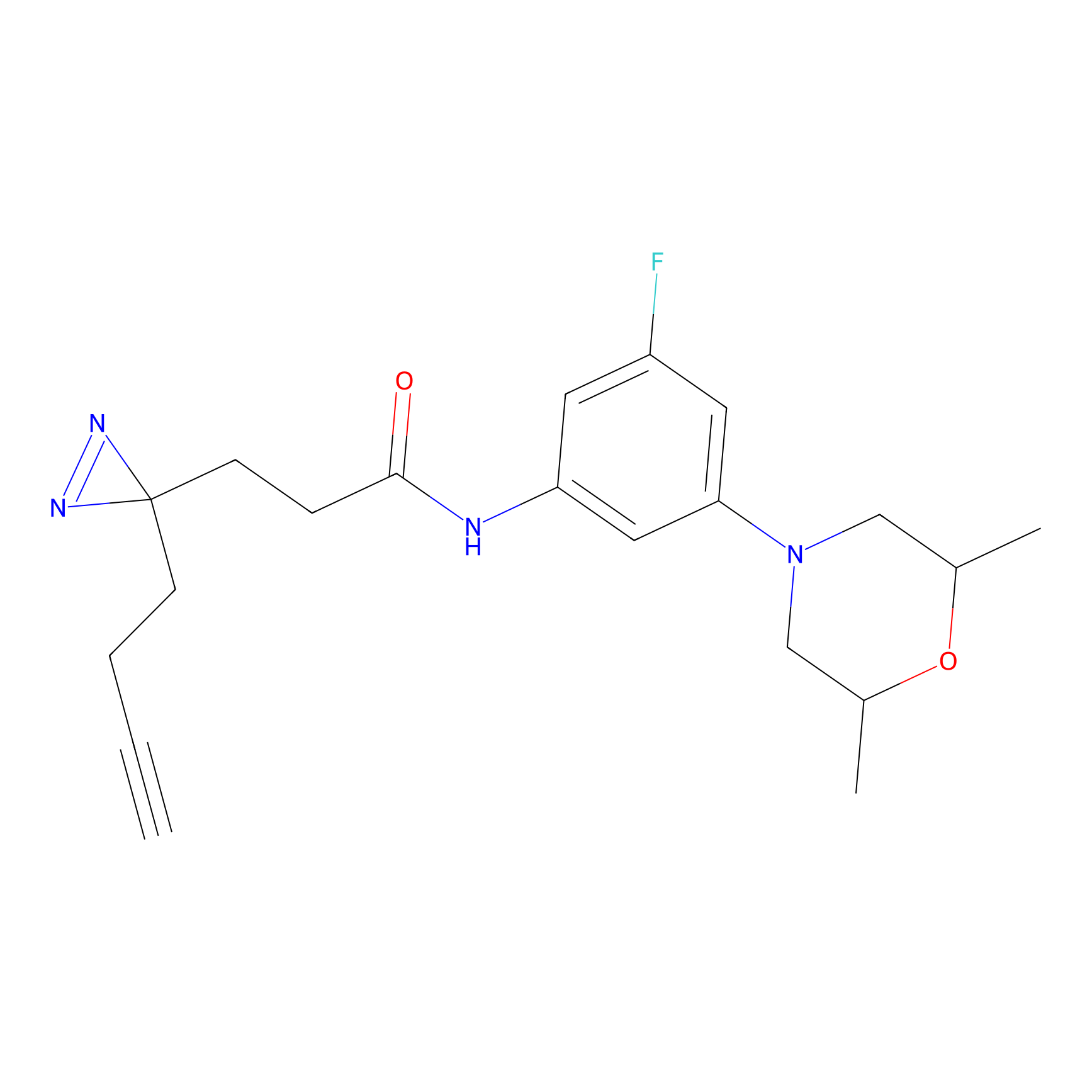
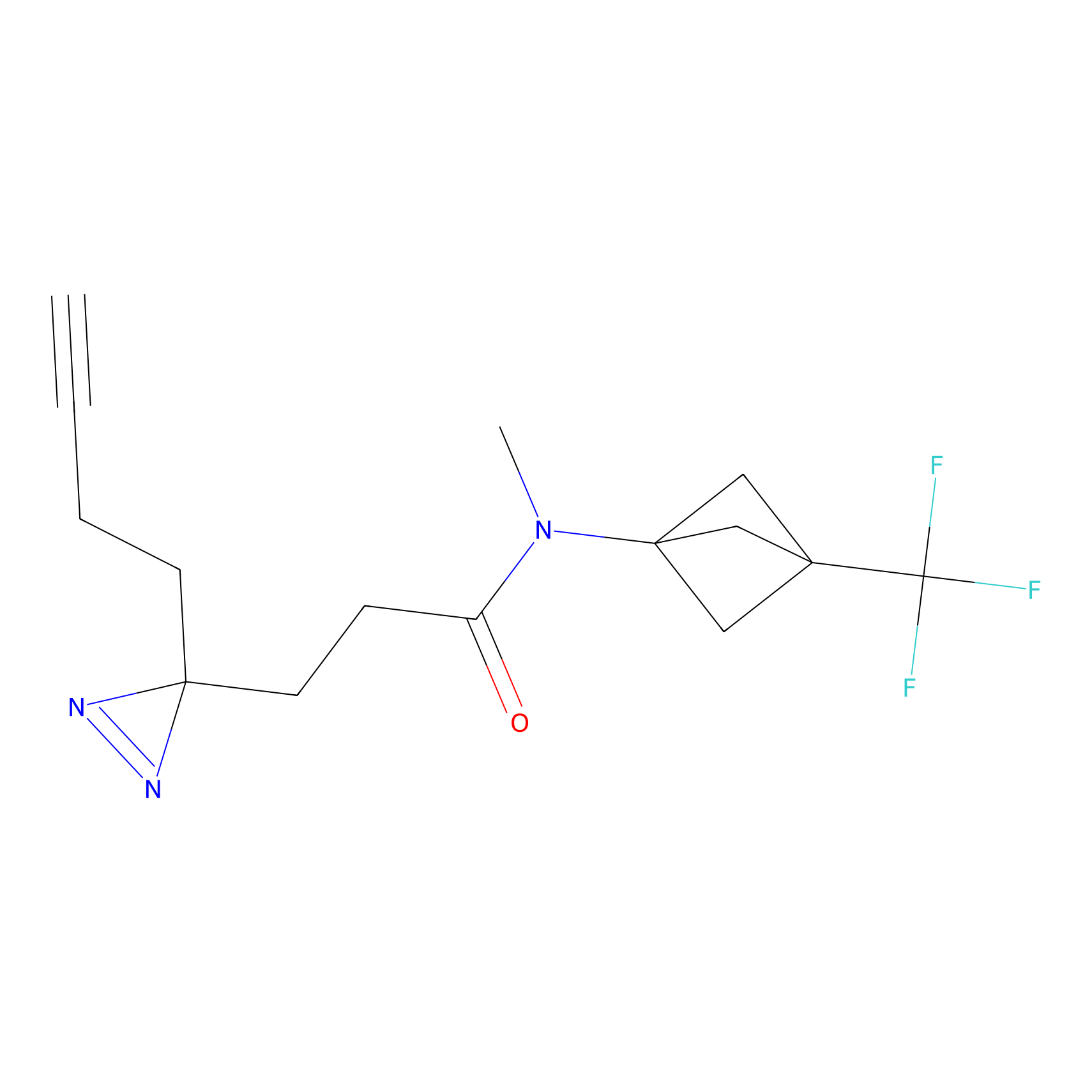
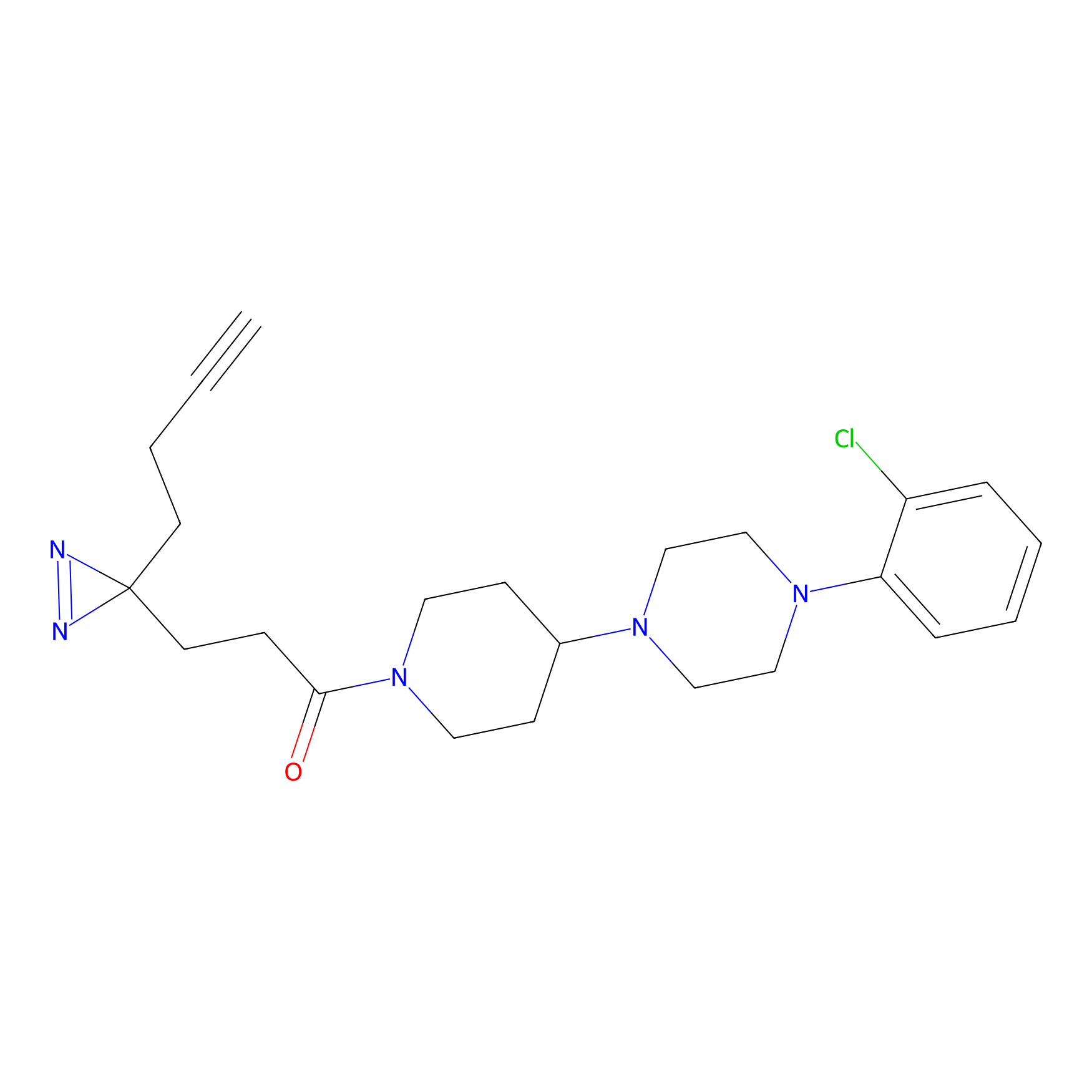
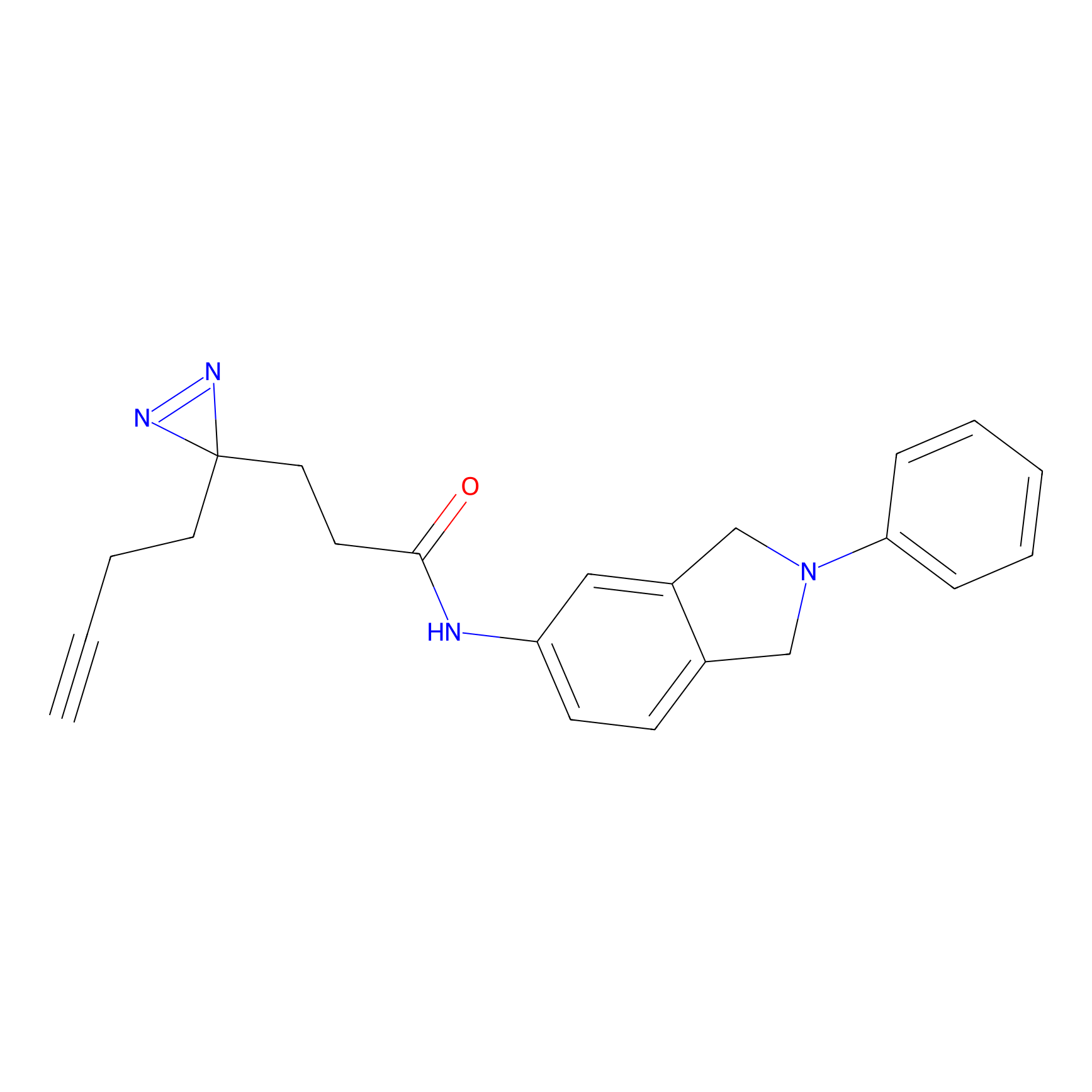
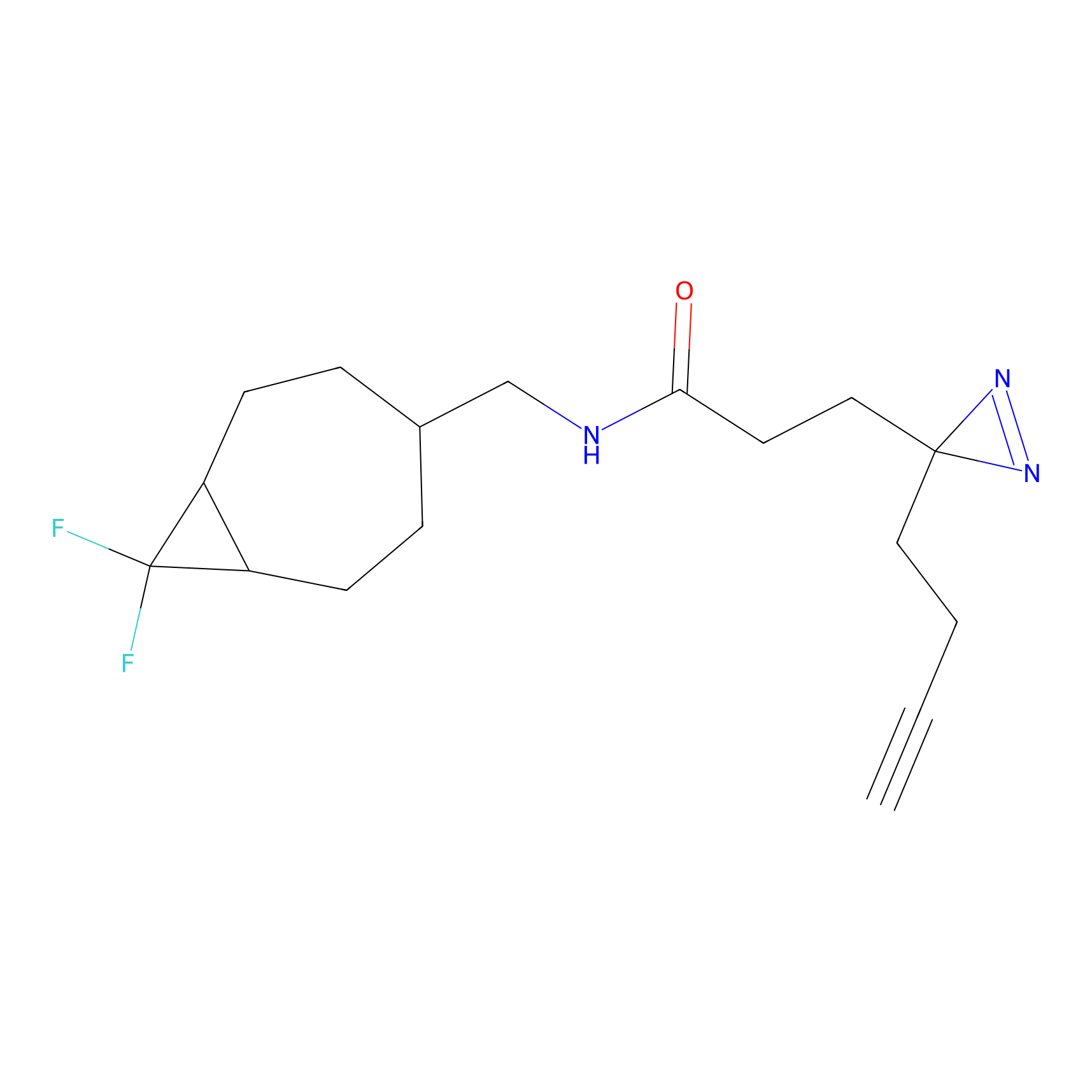
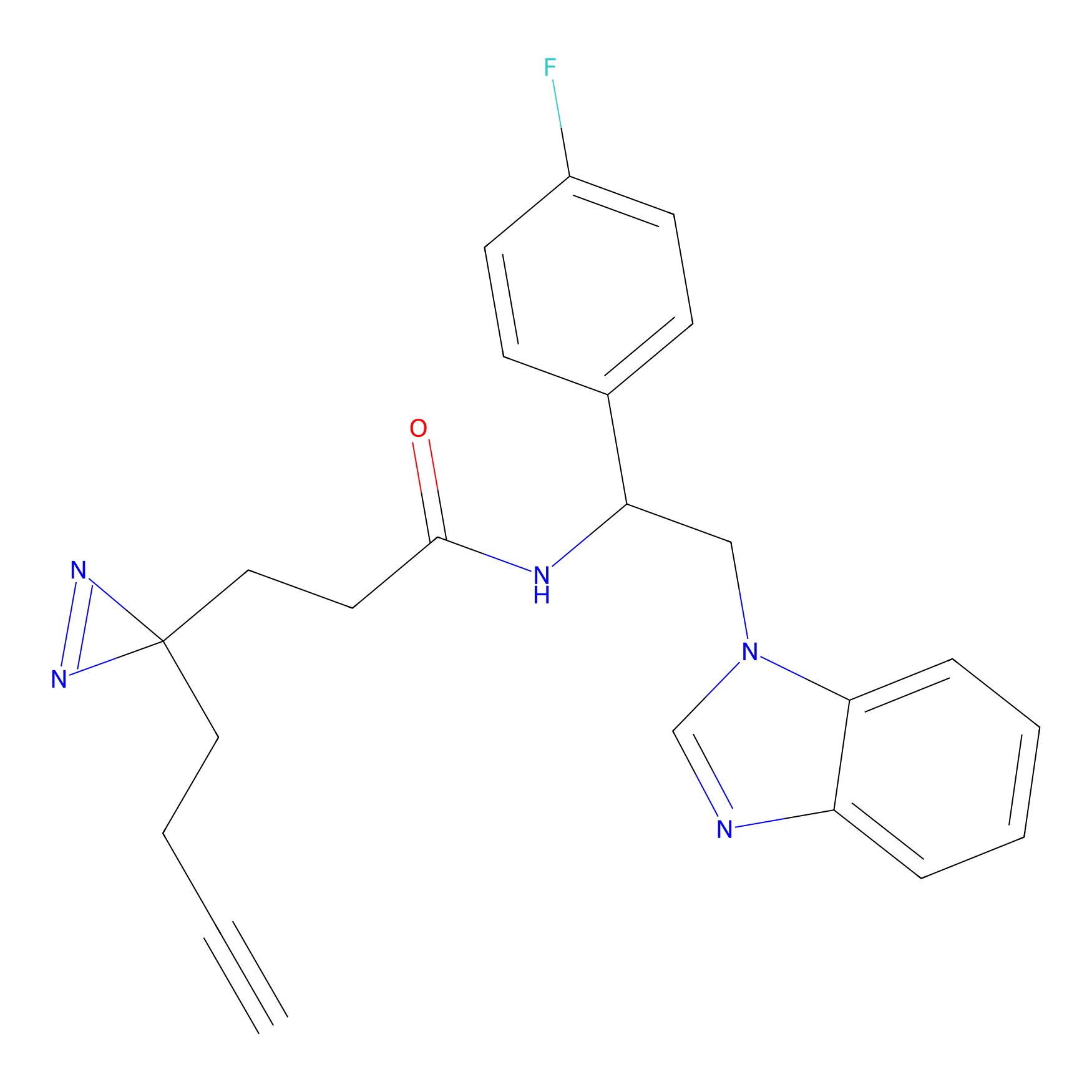
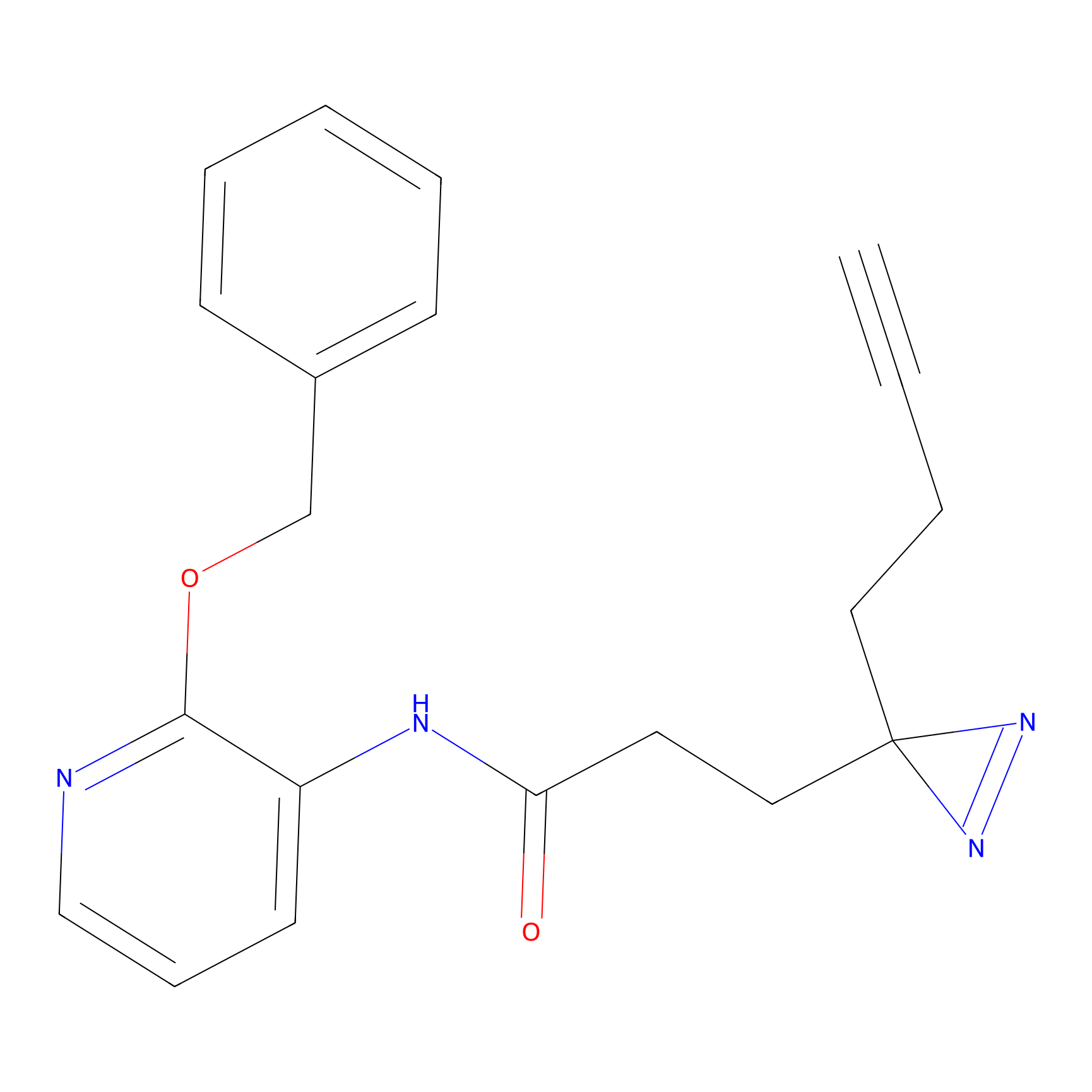
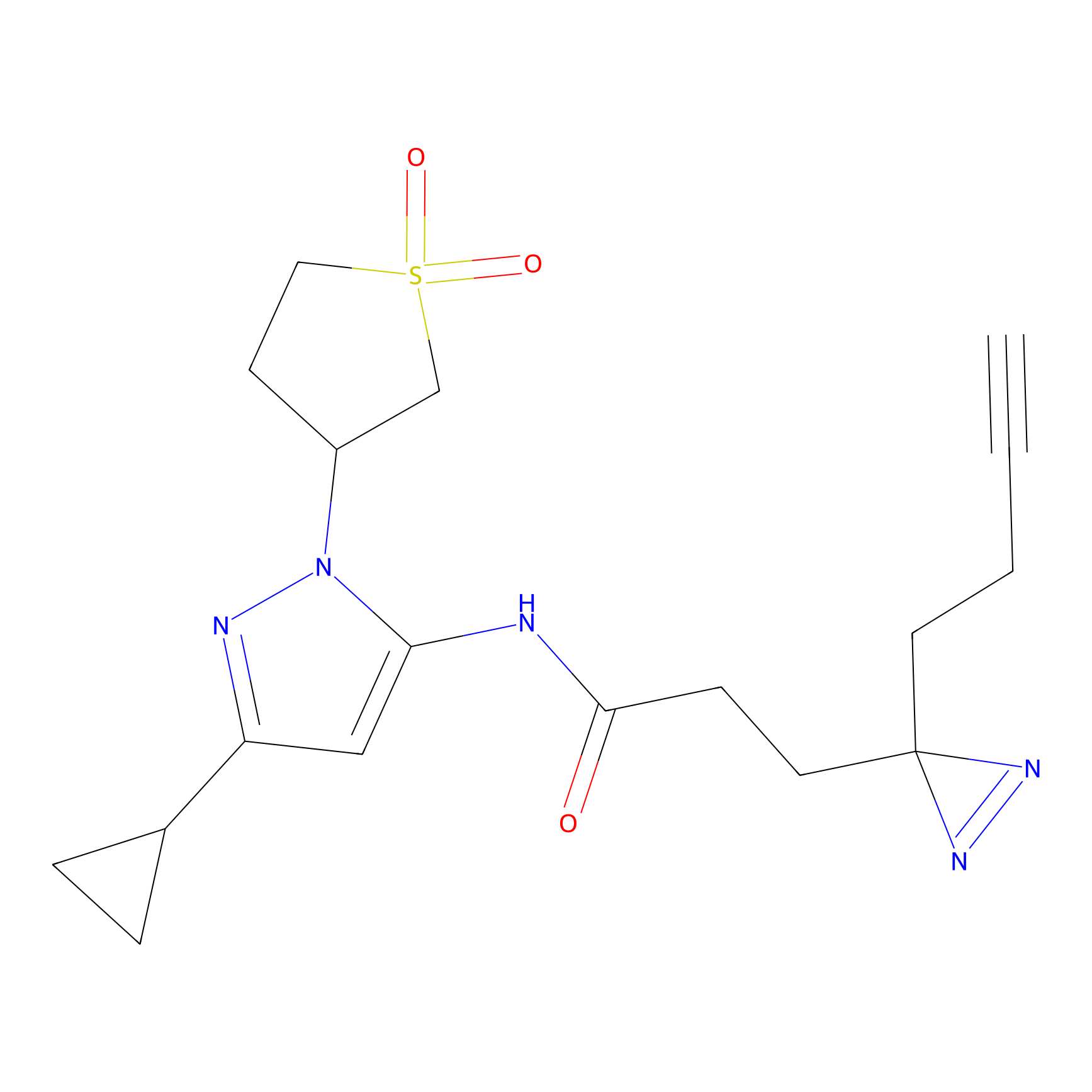
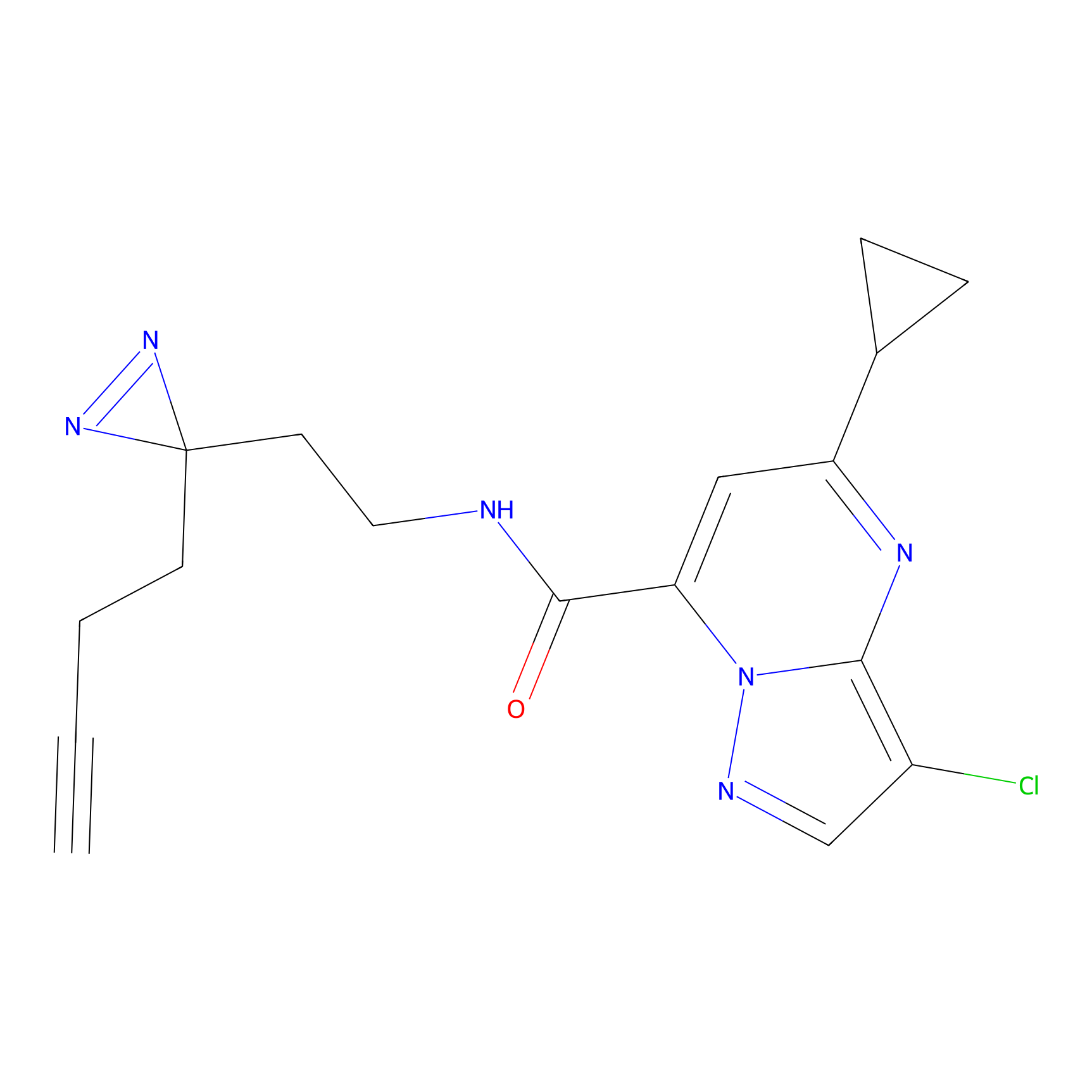
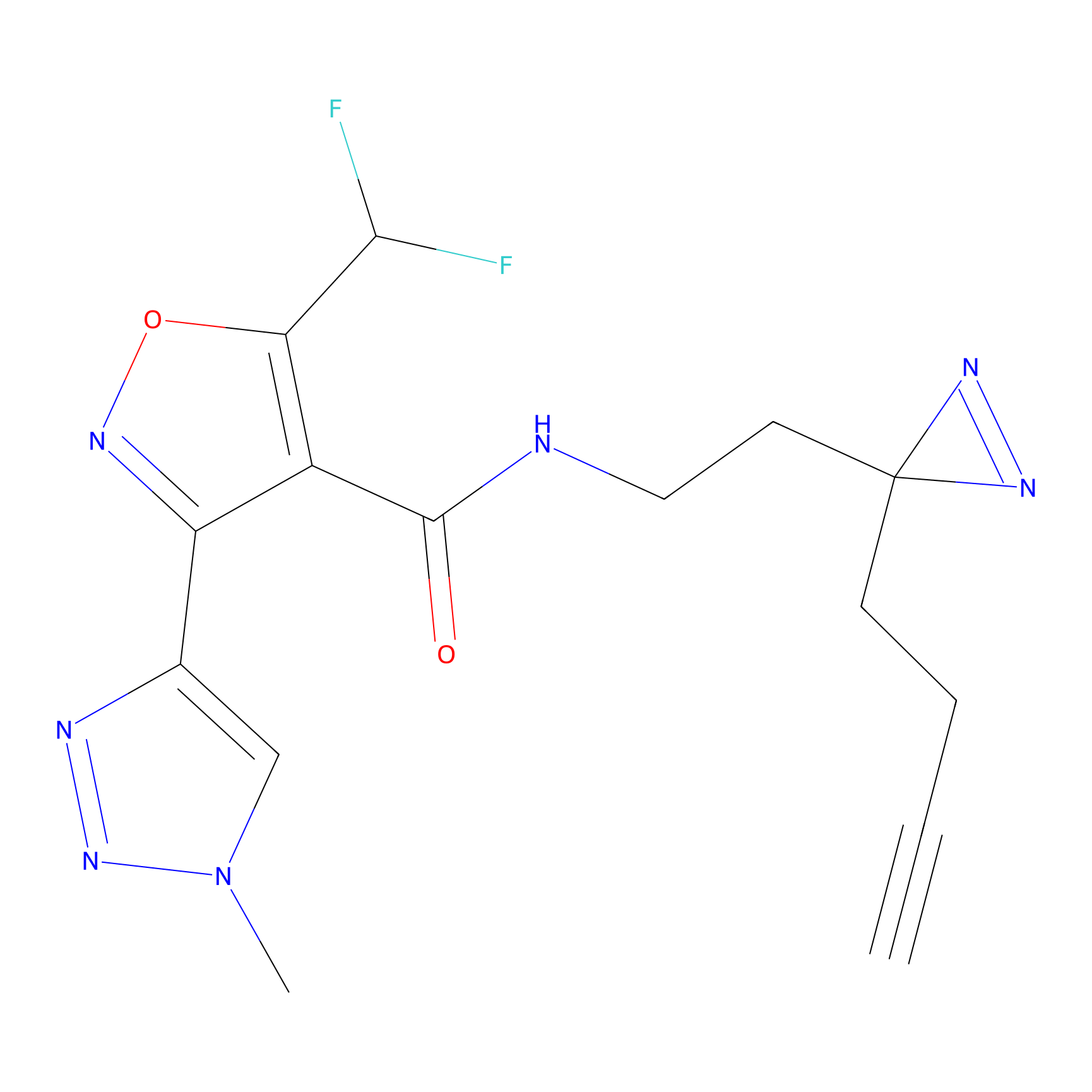
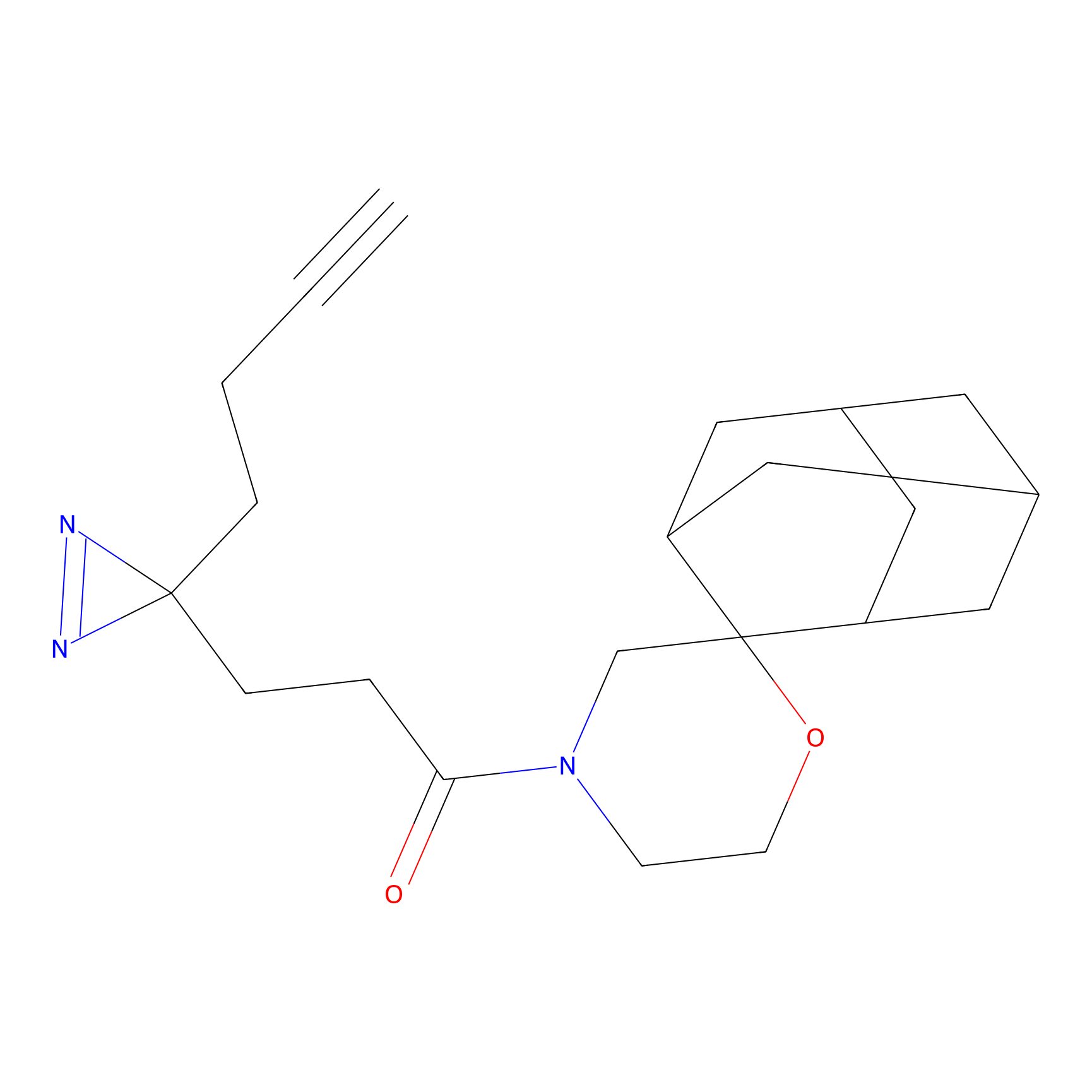
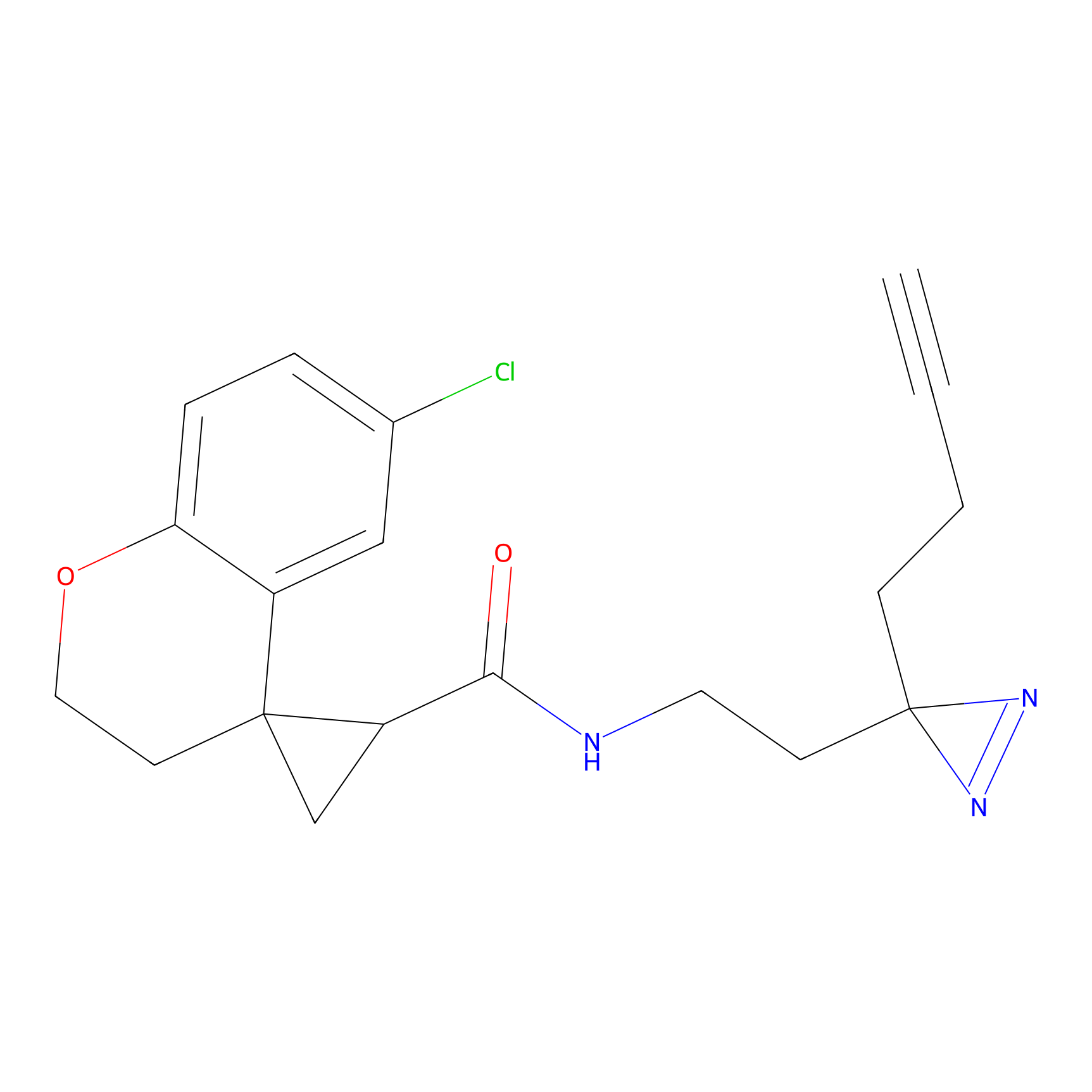
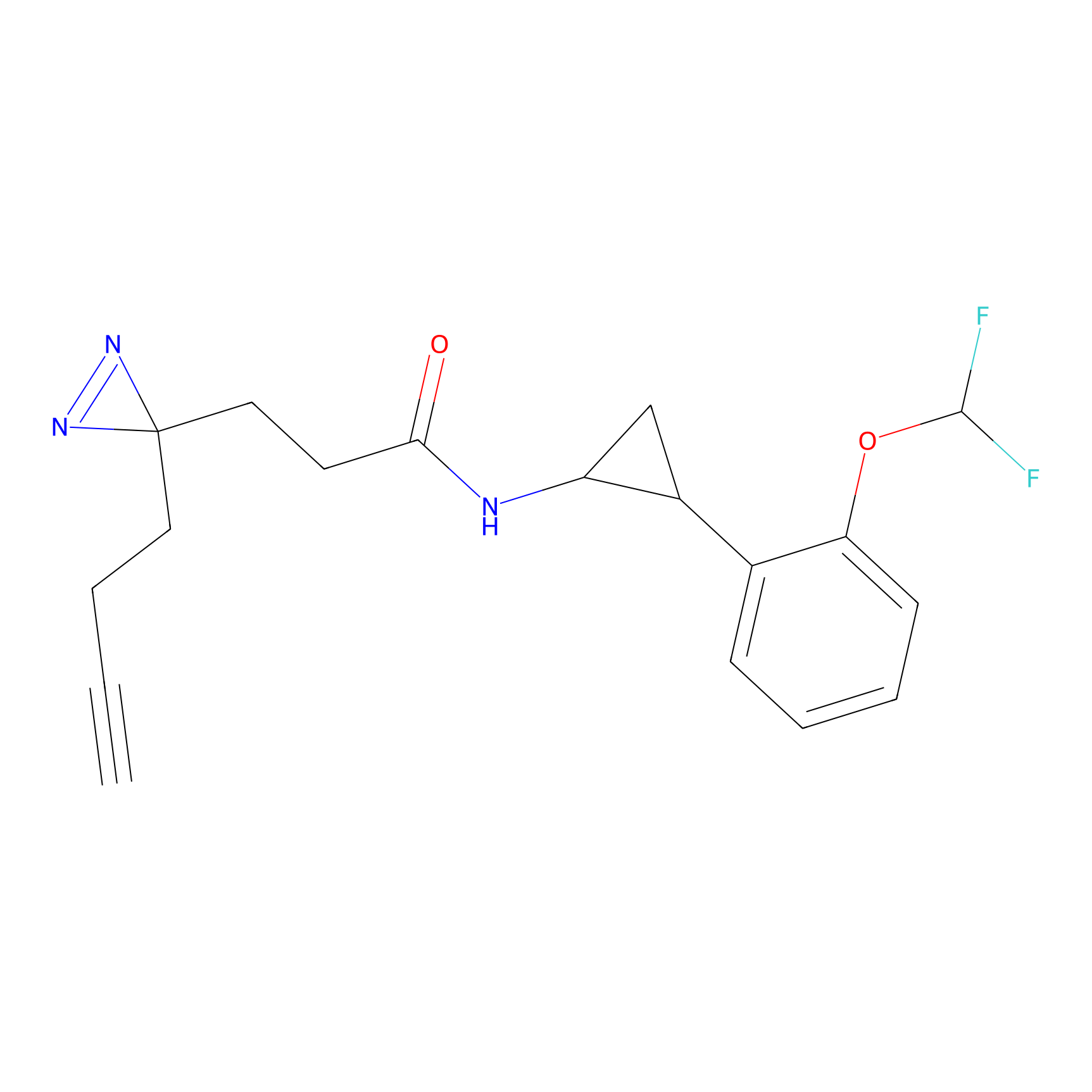
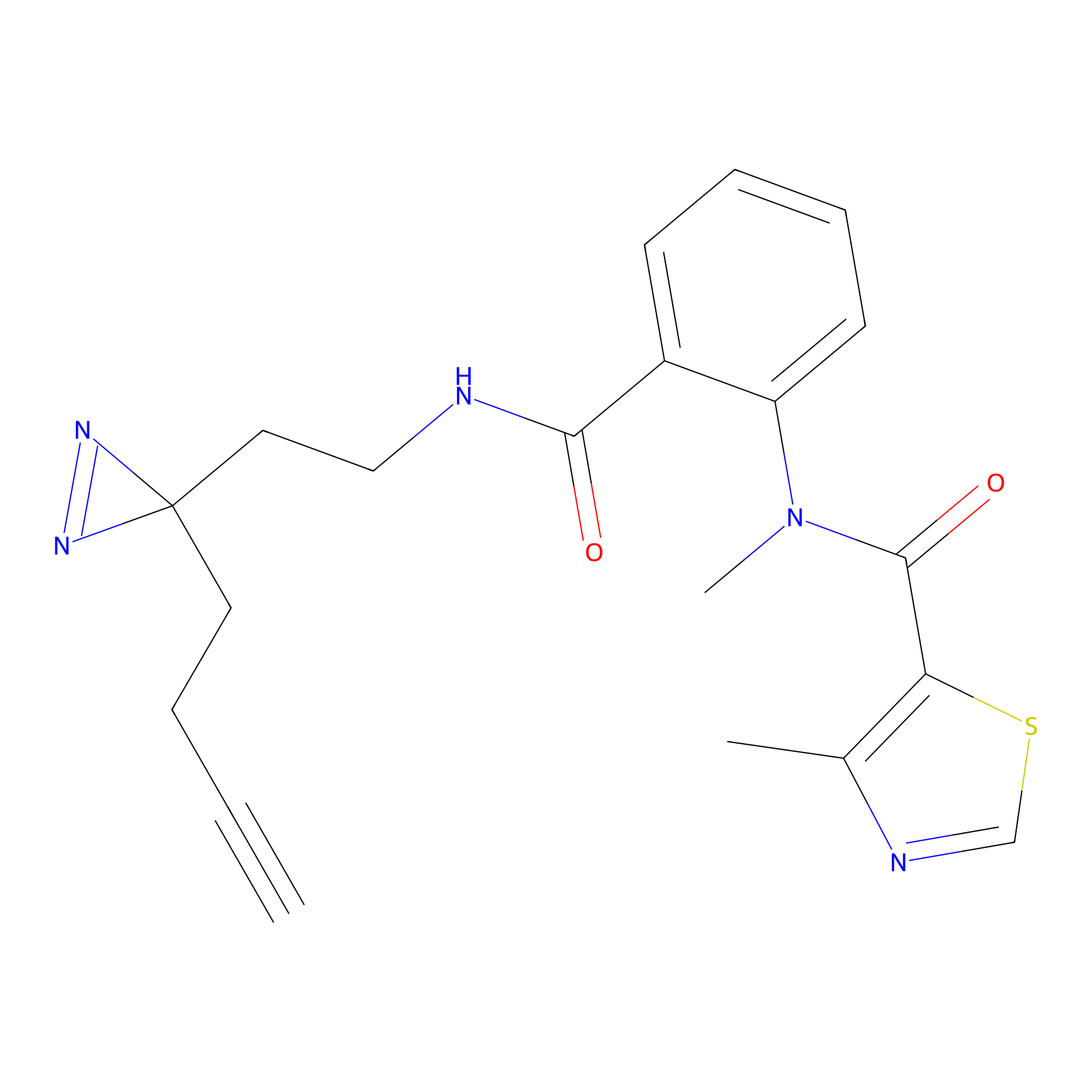
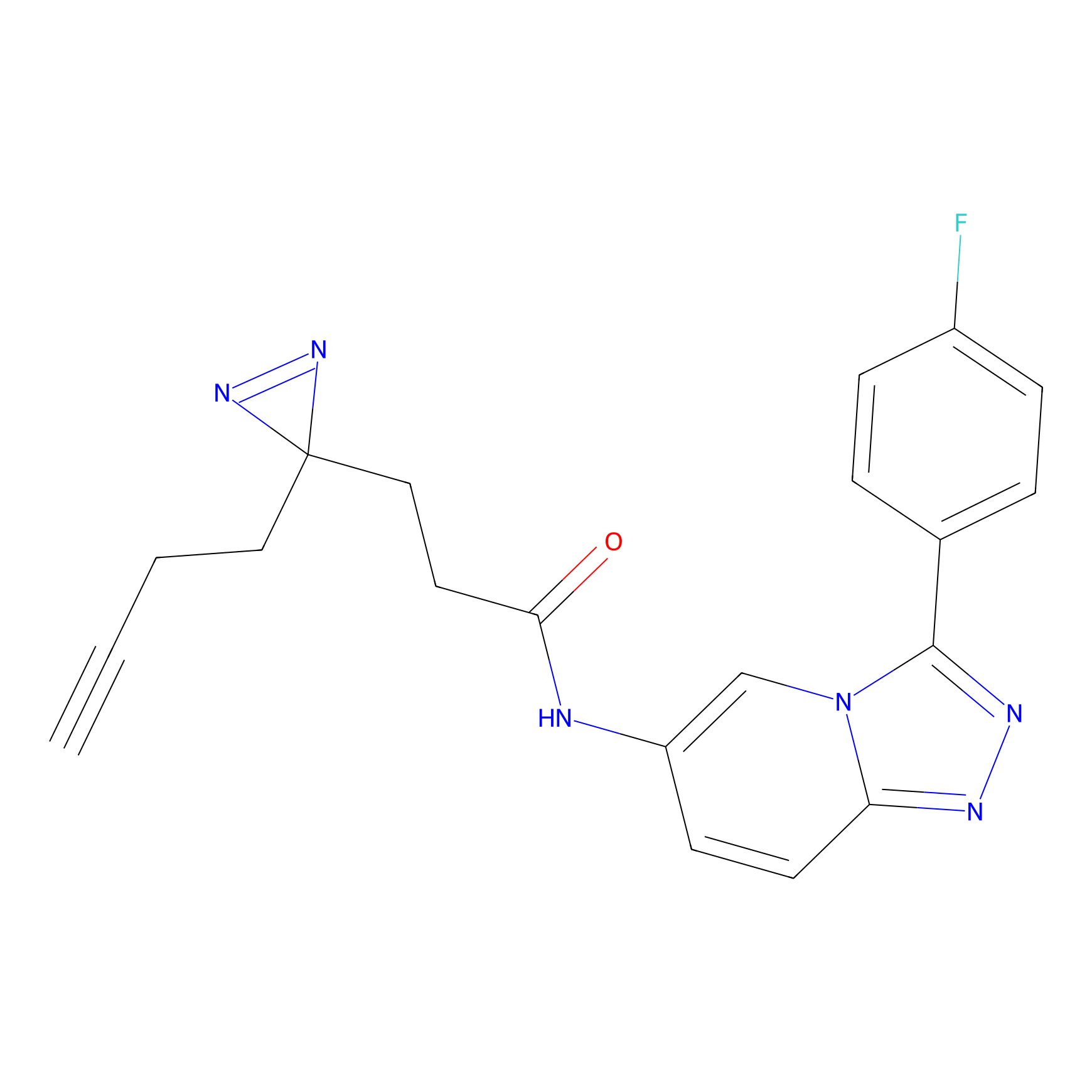
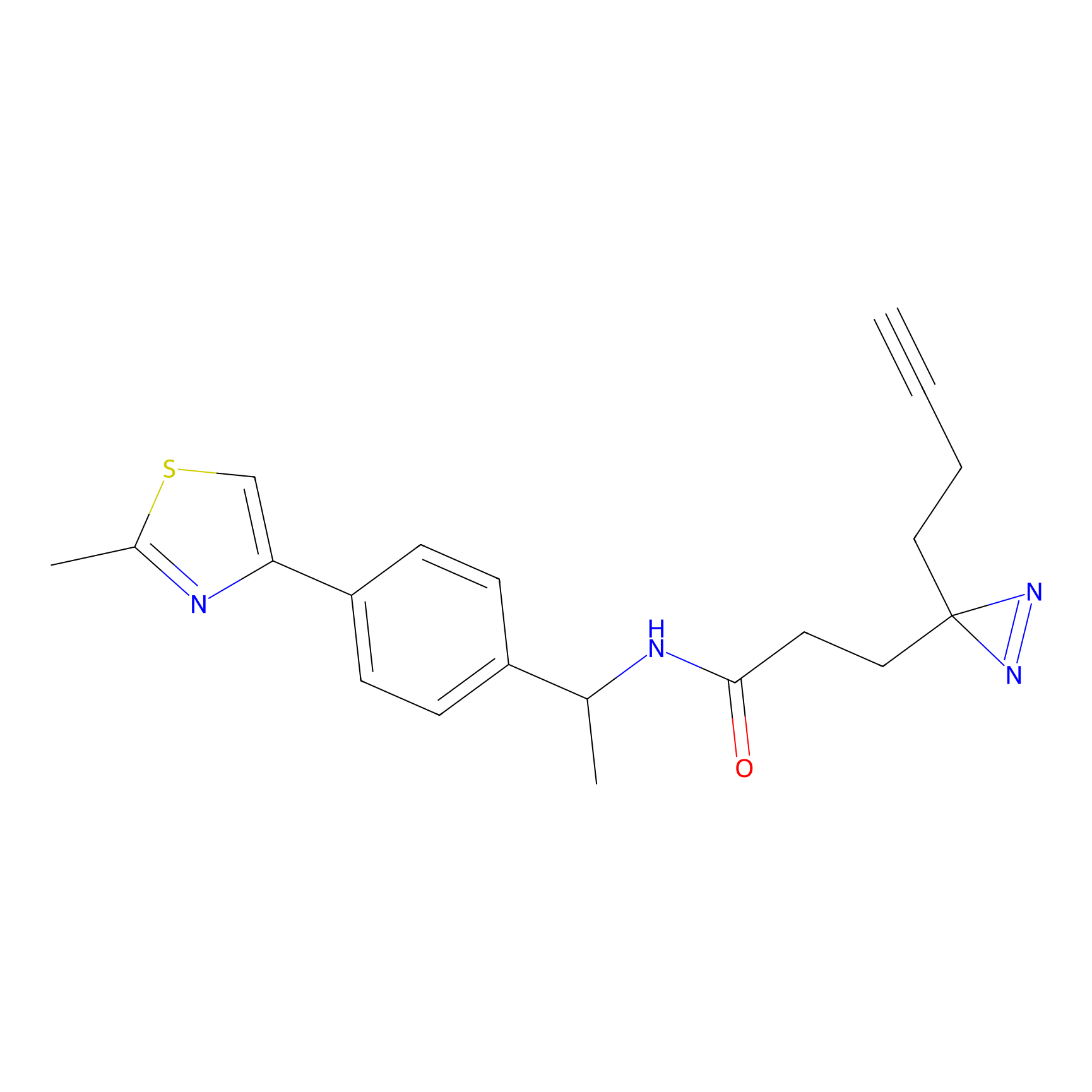
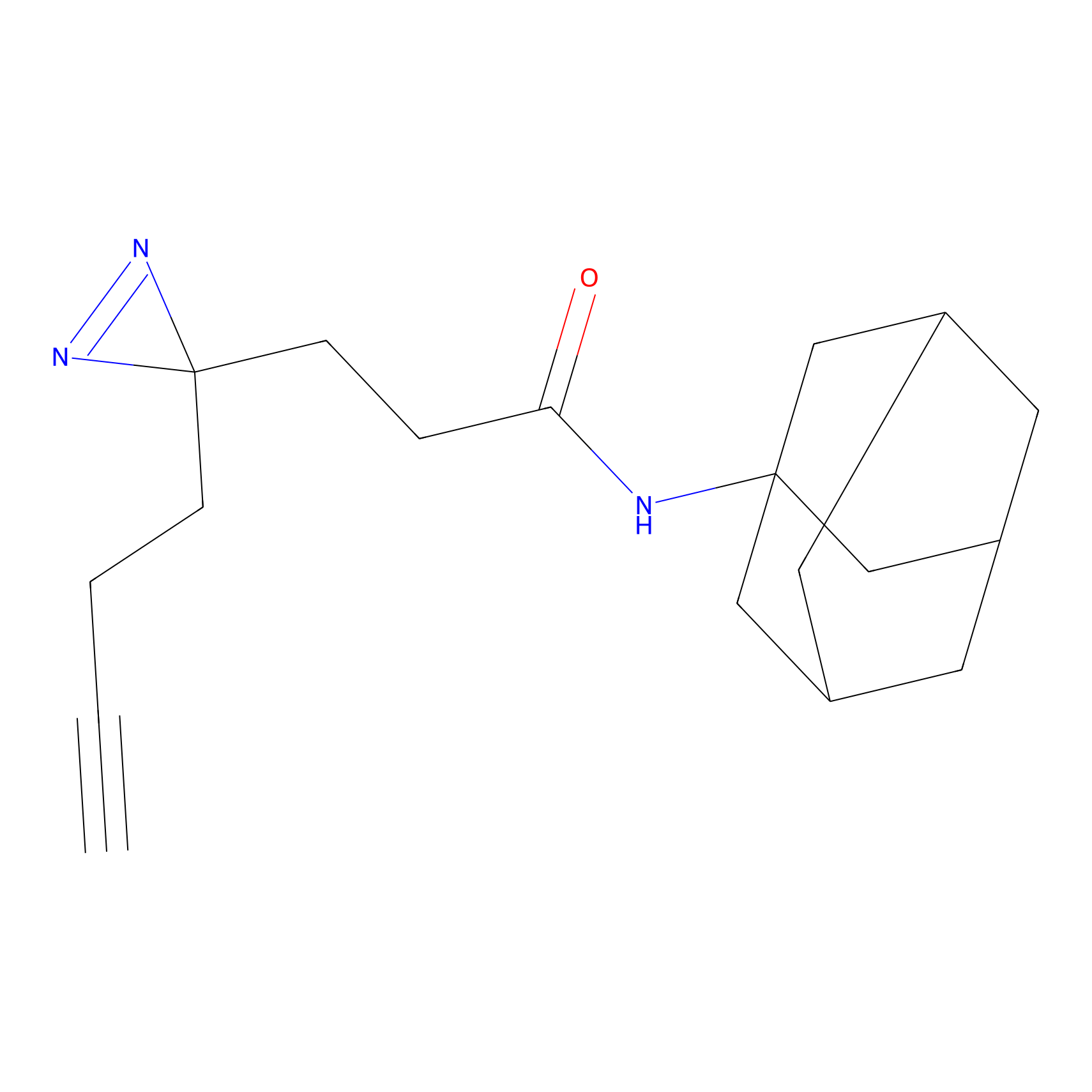
IA-alkyne Probe Info |
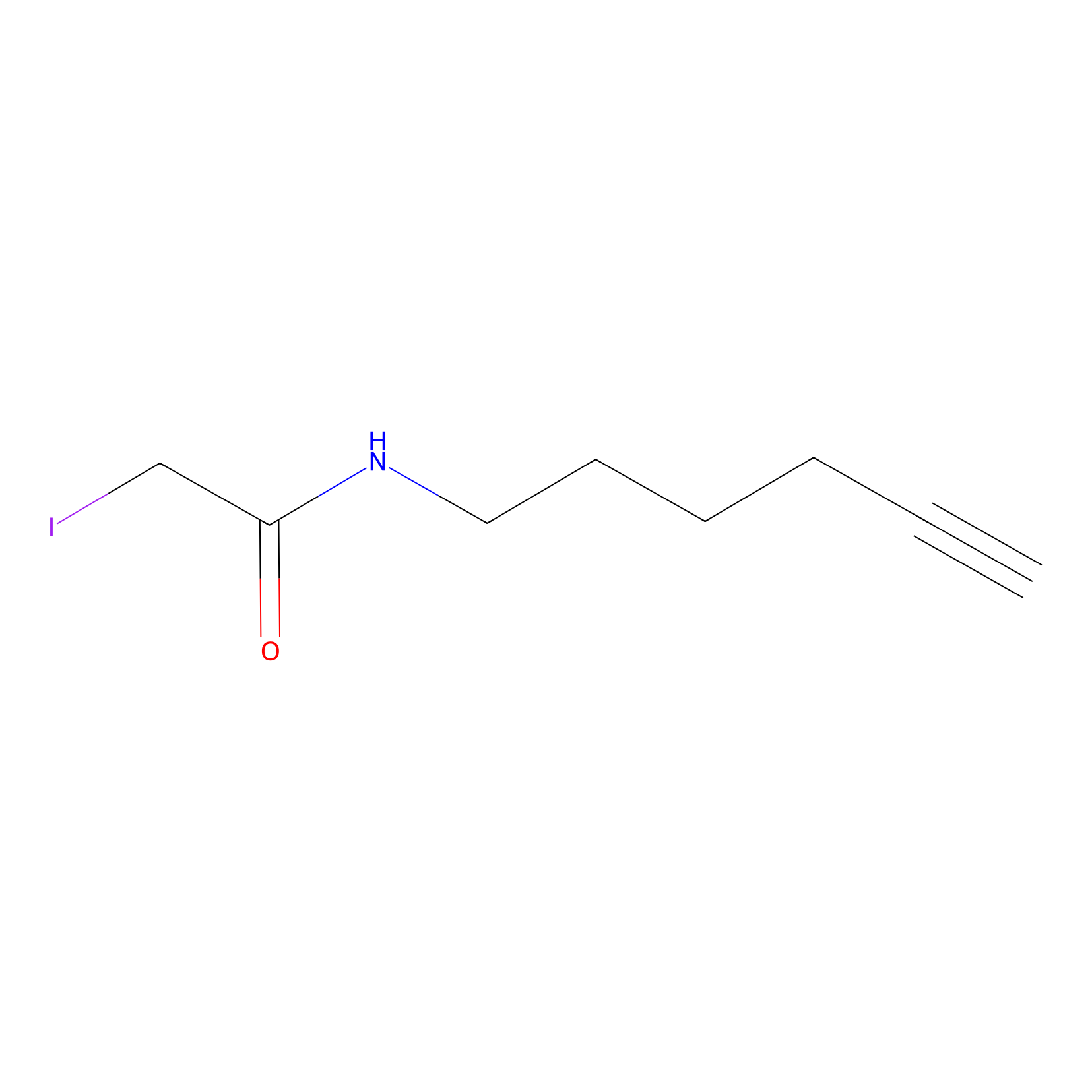 |
C22(1.33) | LDD2206 | [2] | |
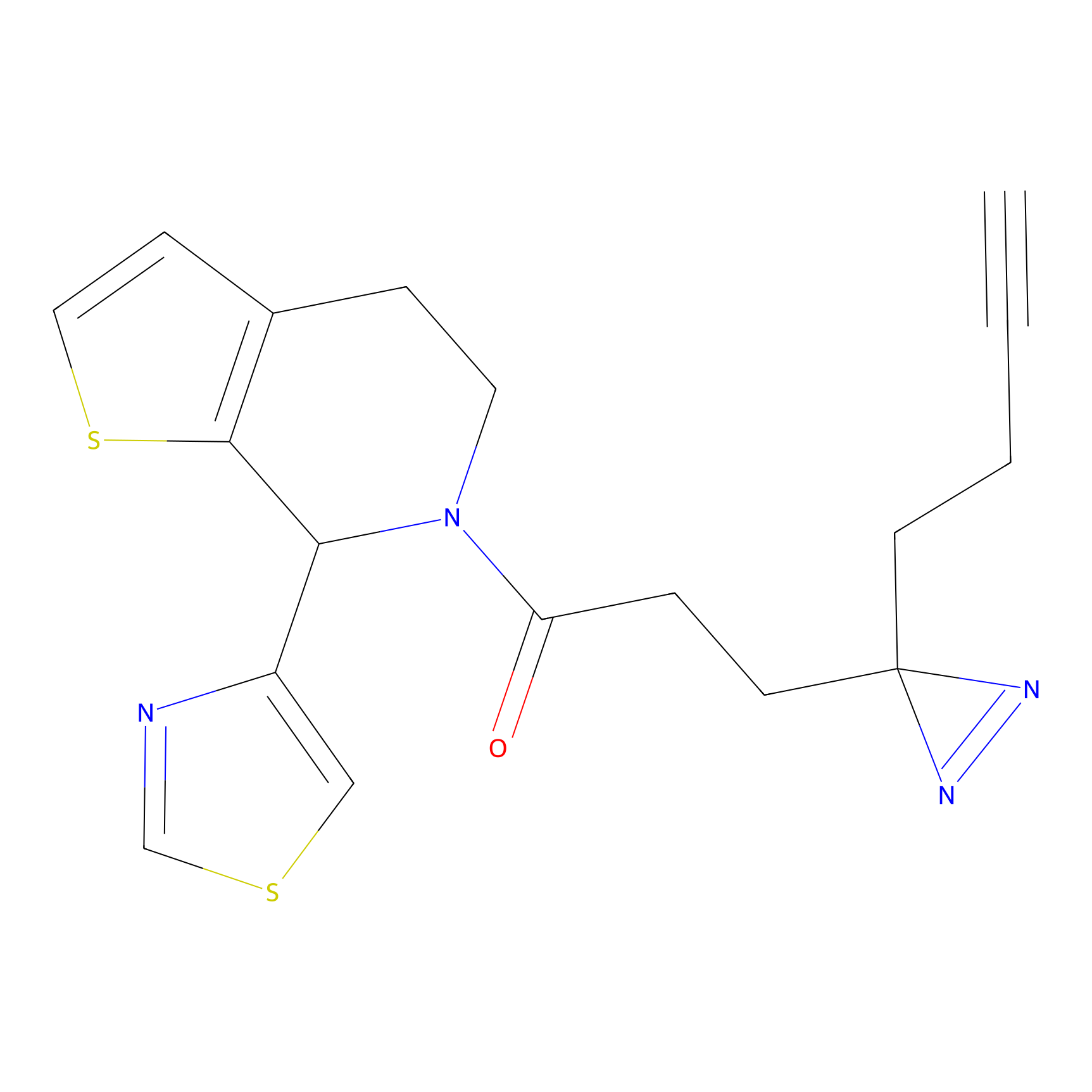
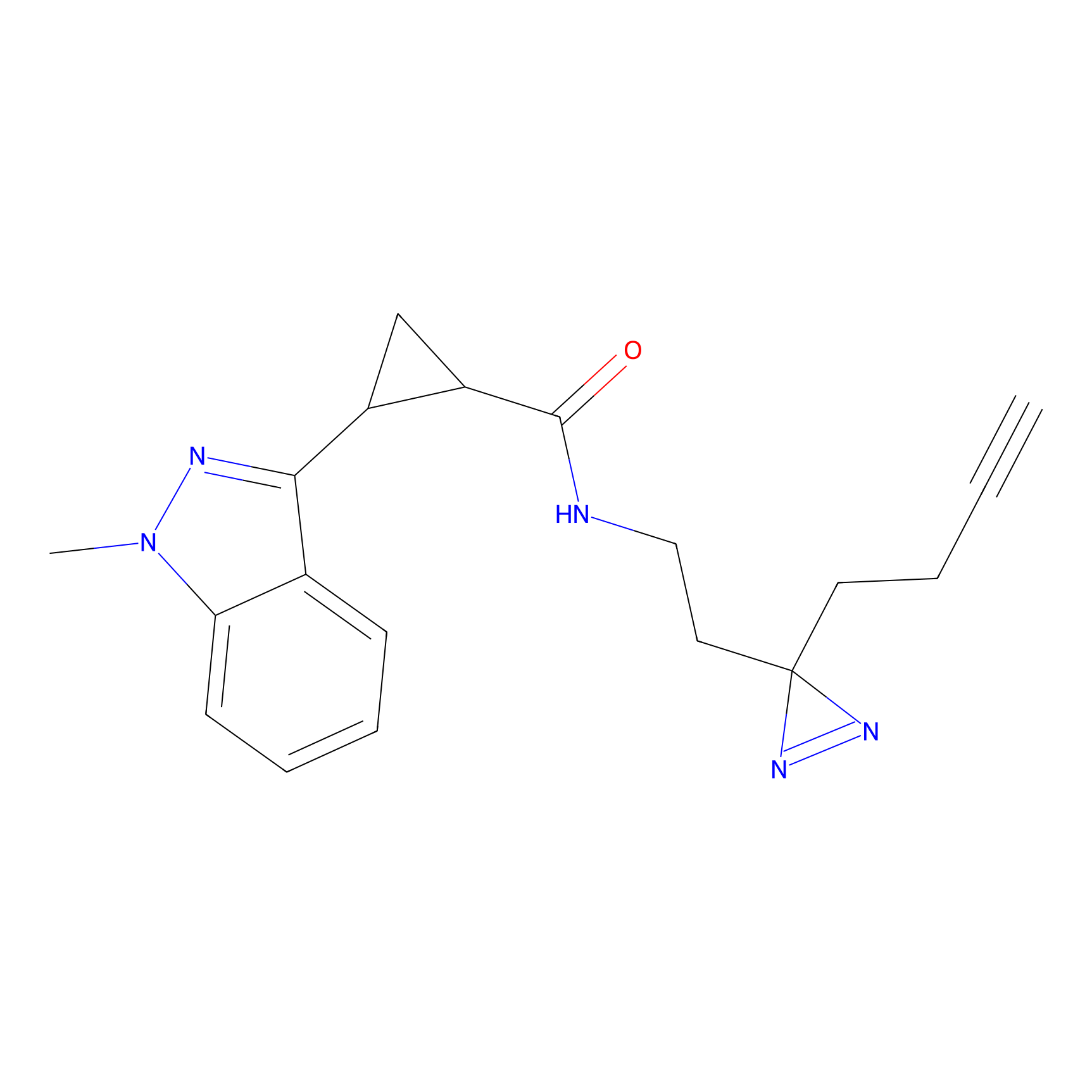
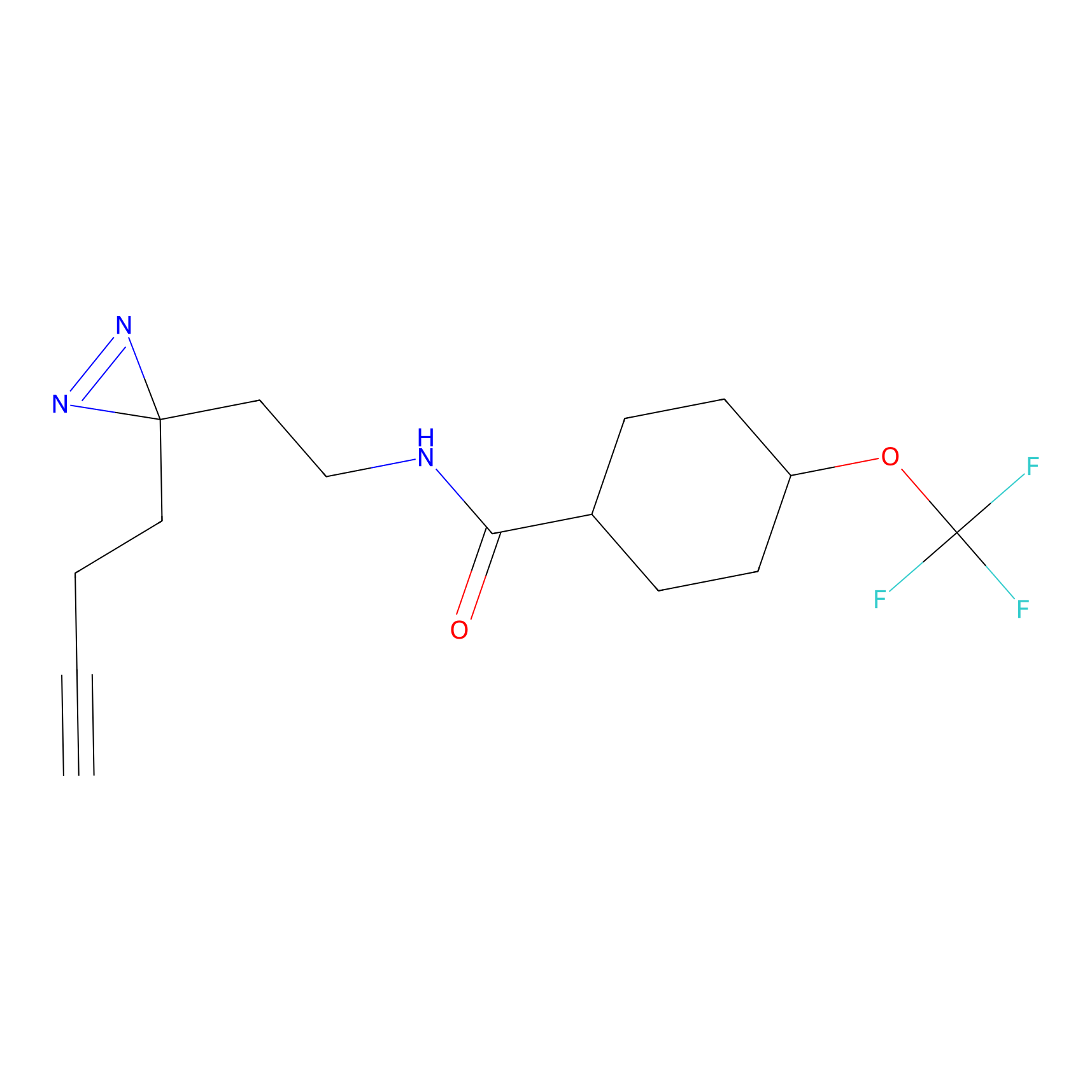
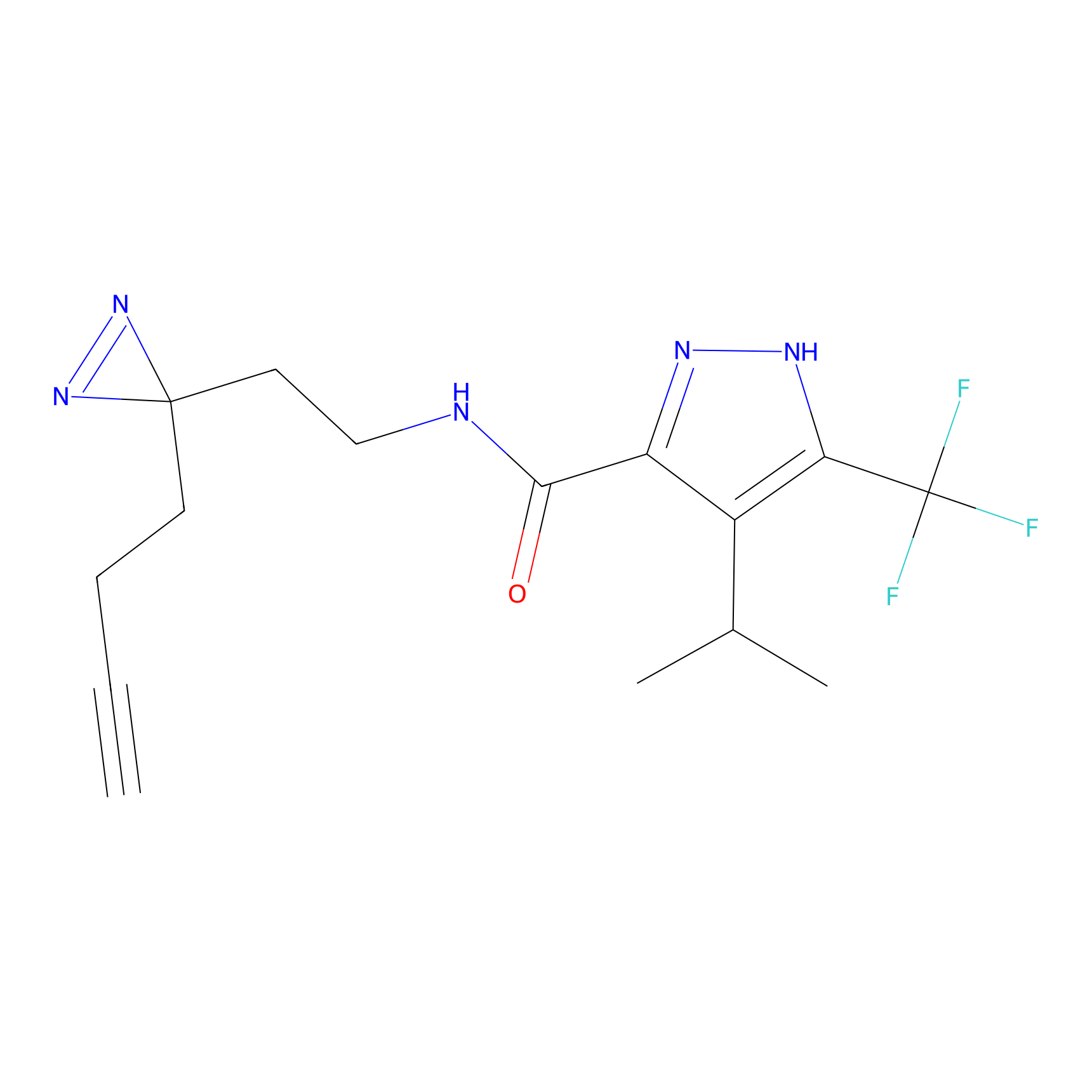
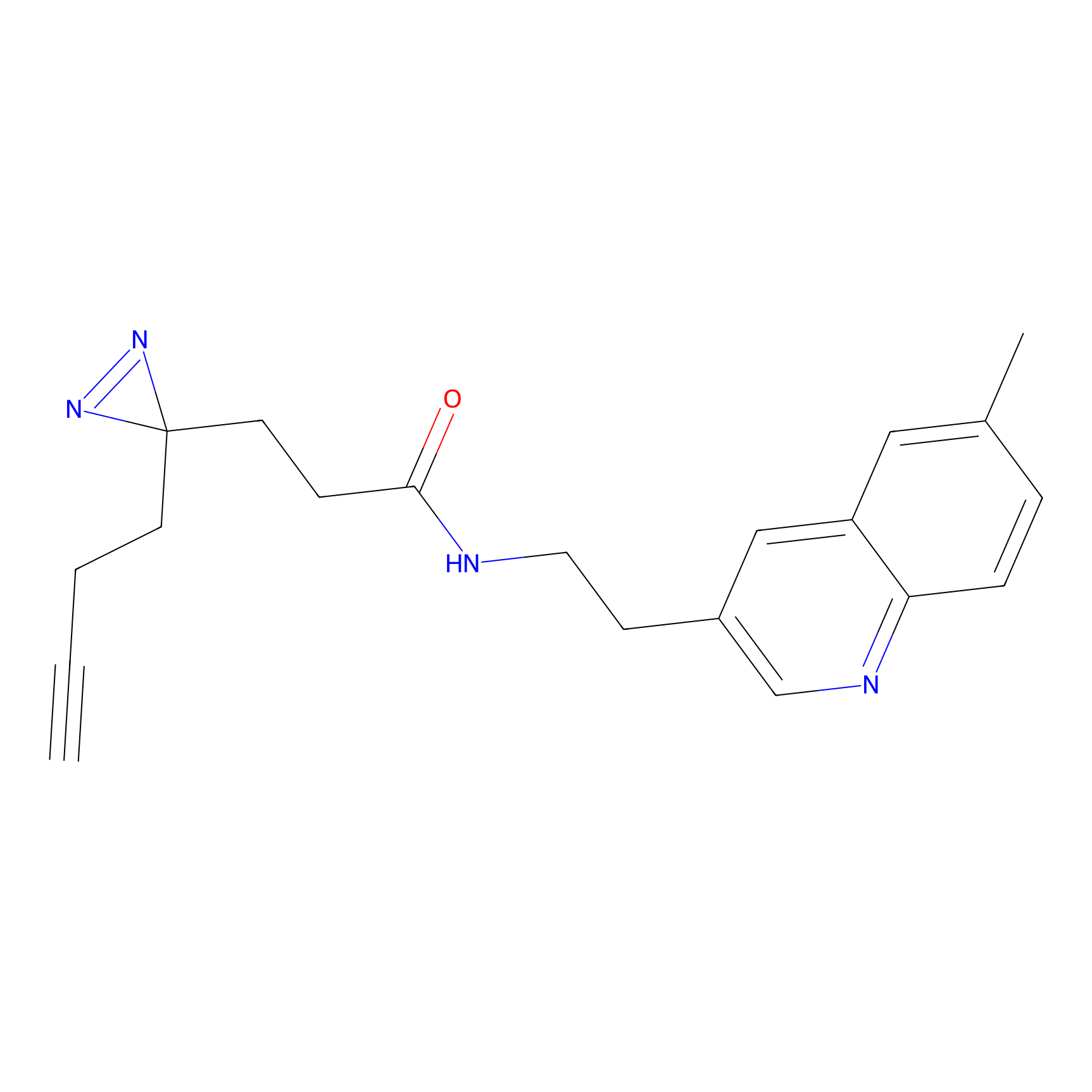
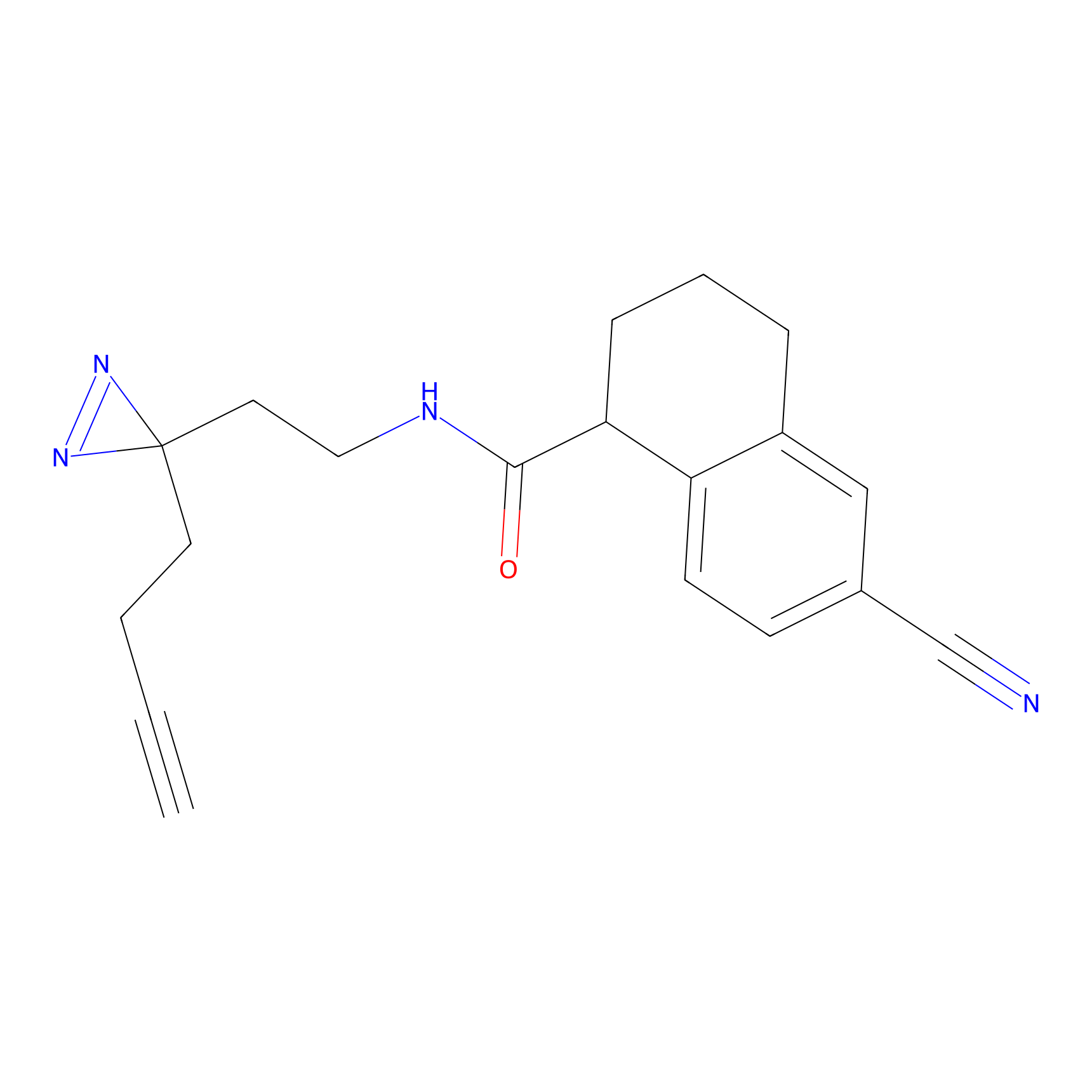
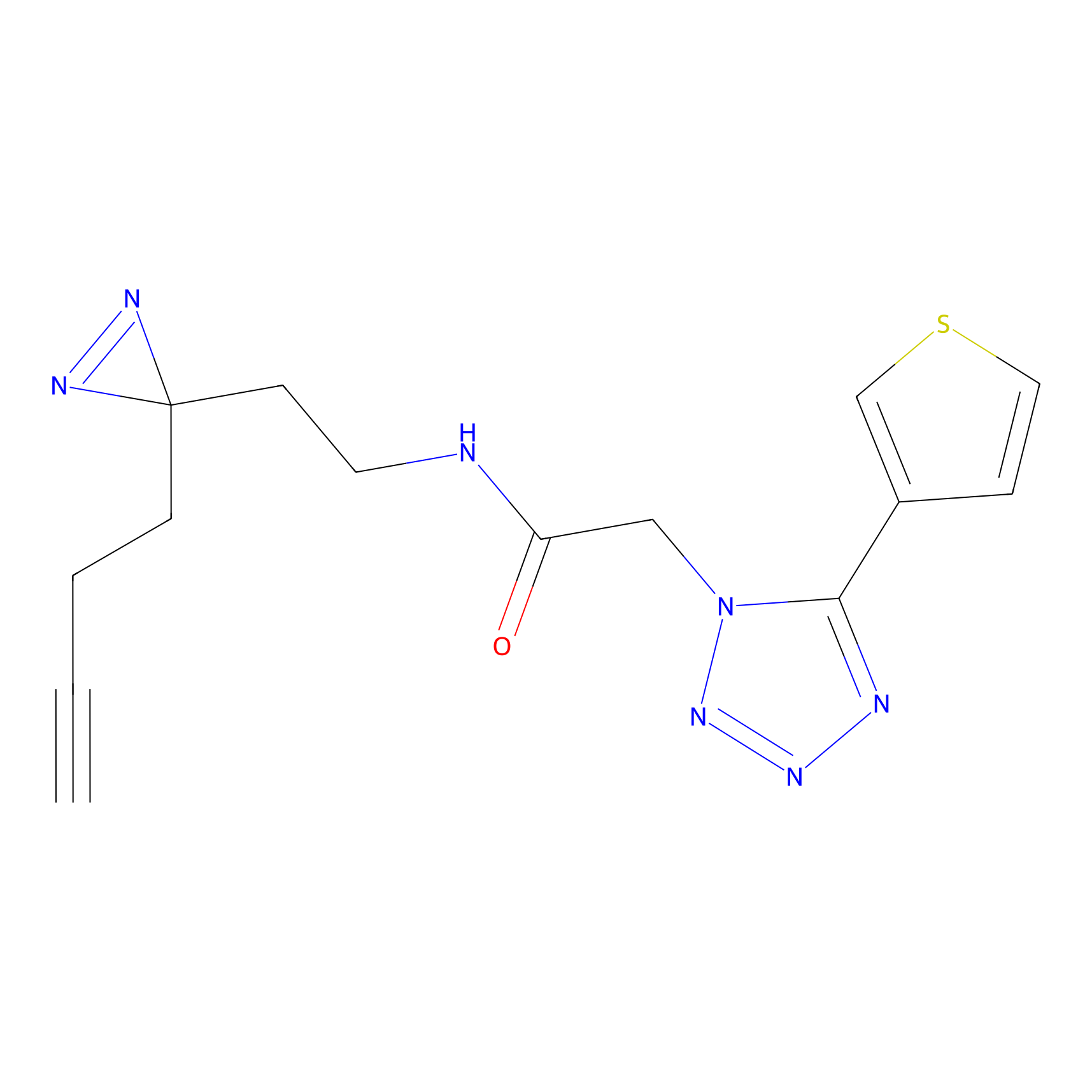
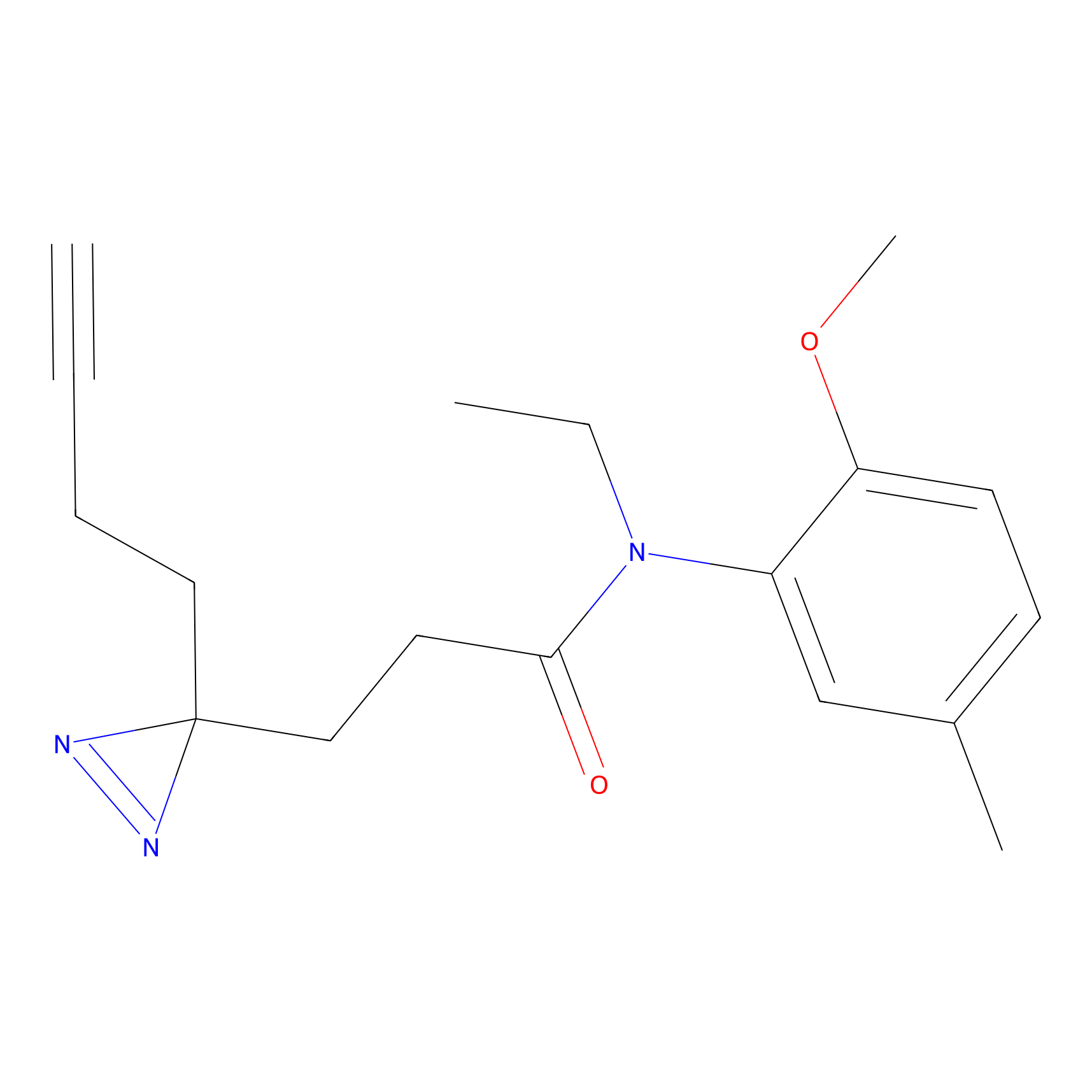
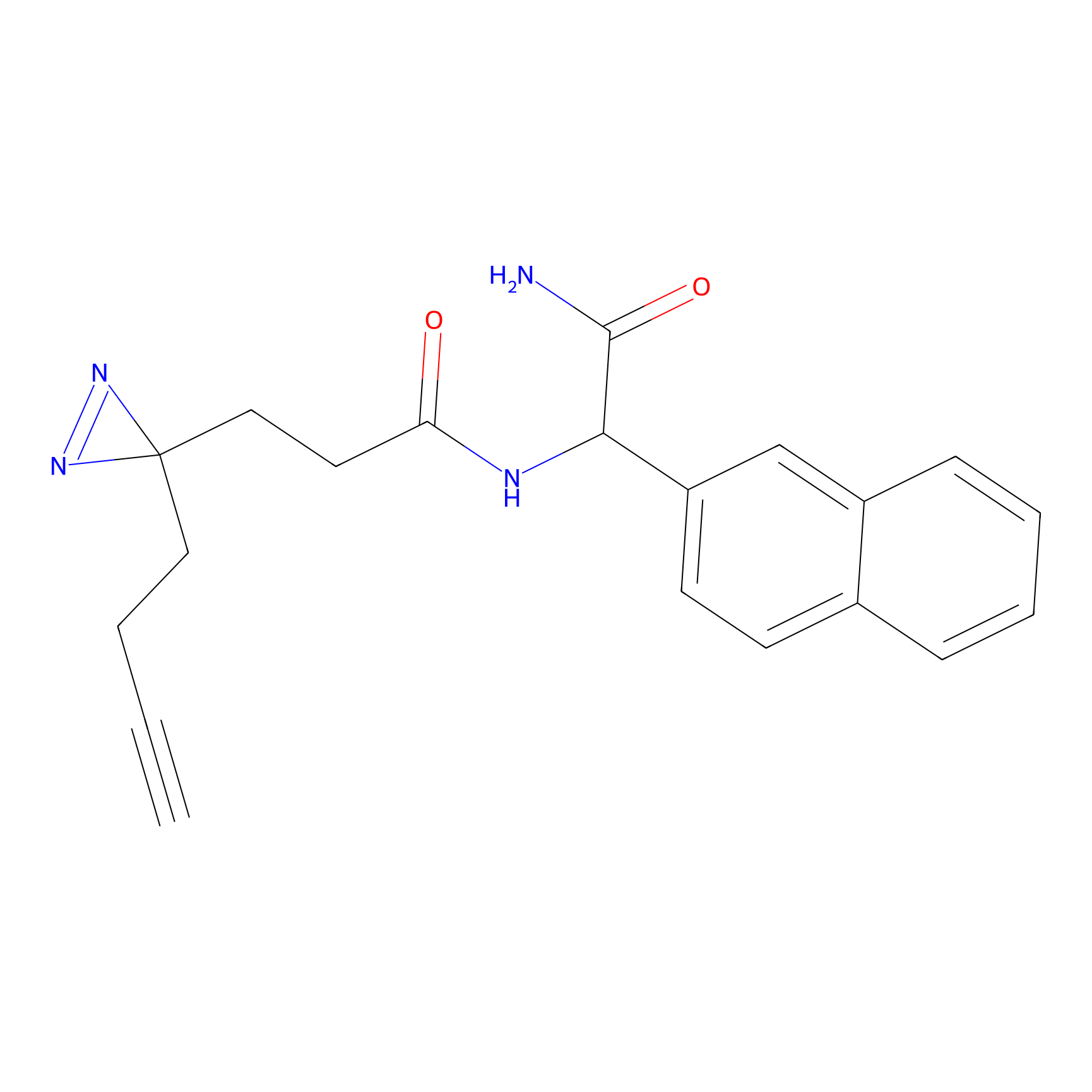
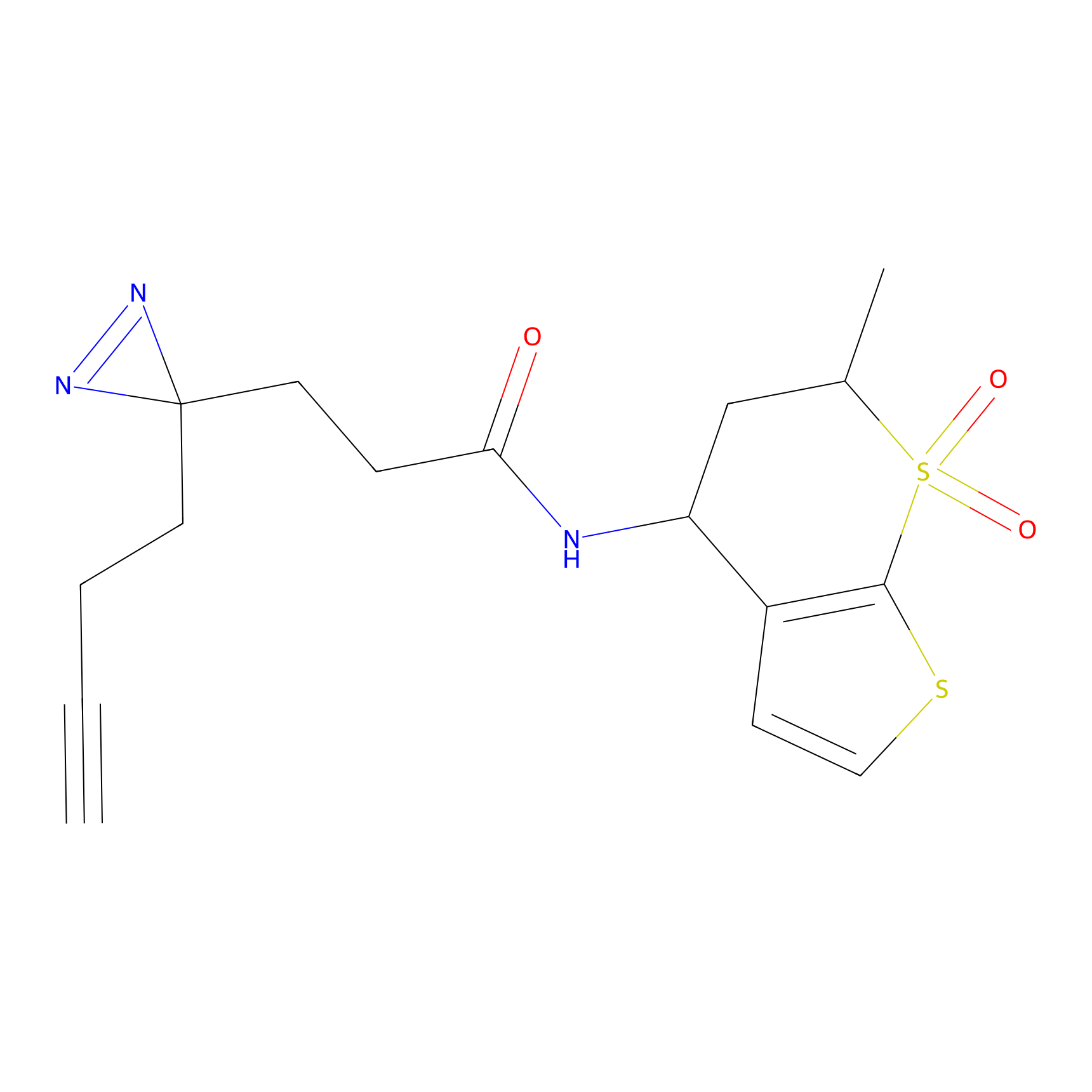
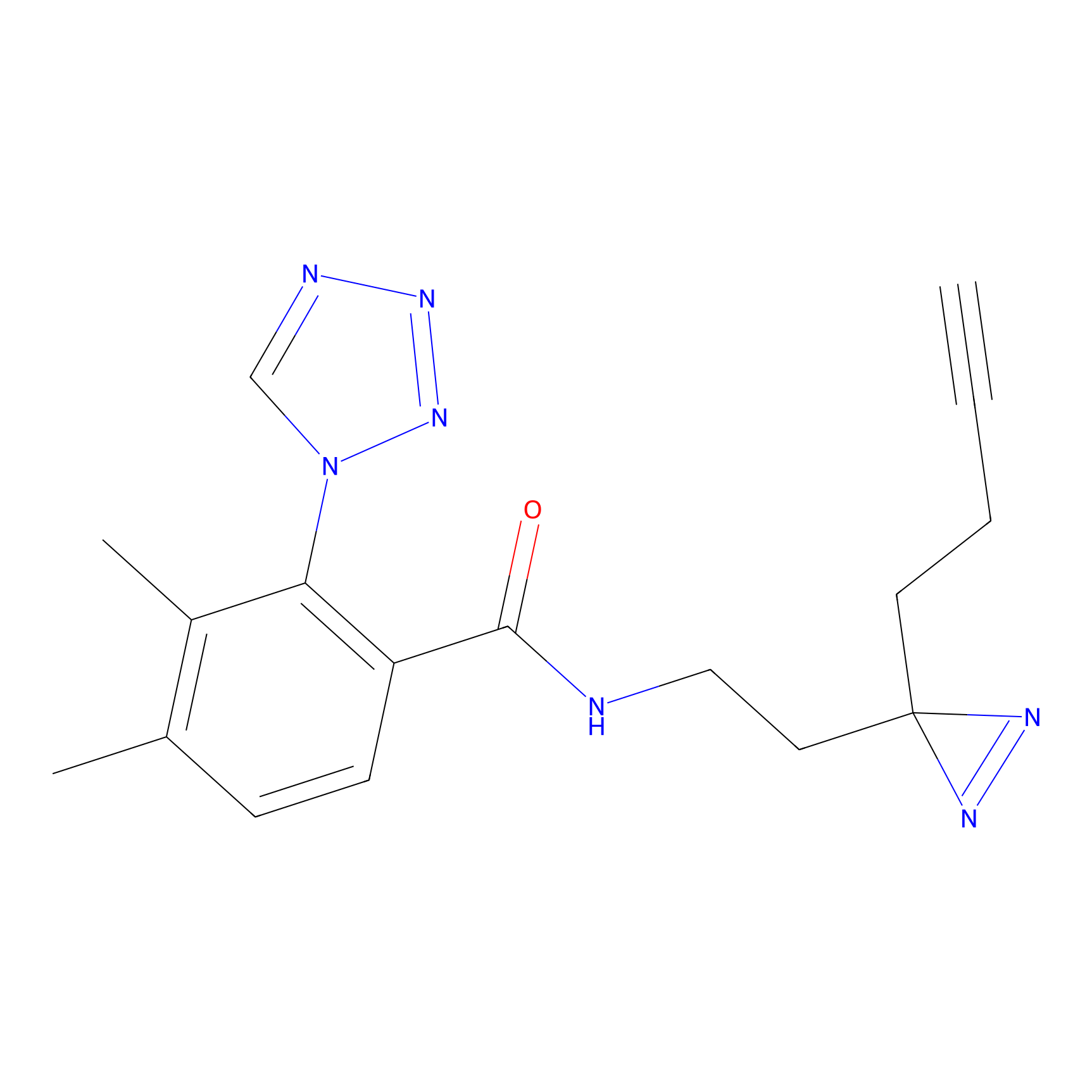
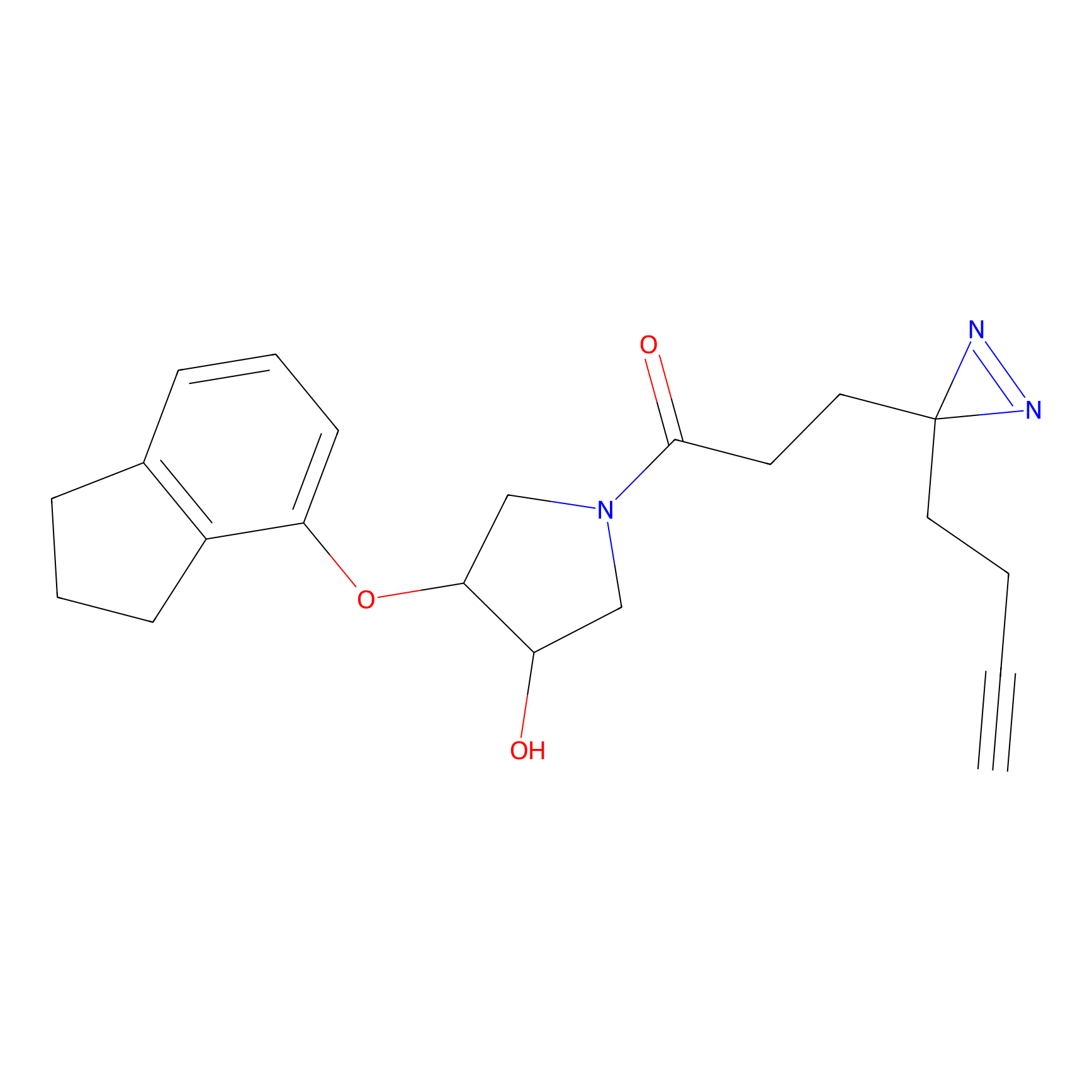
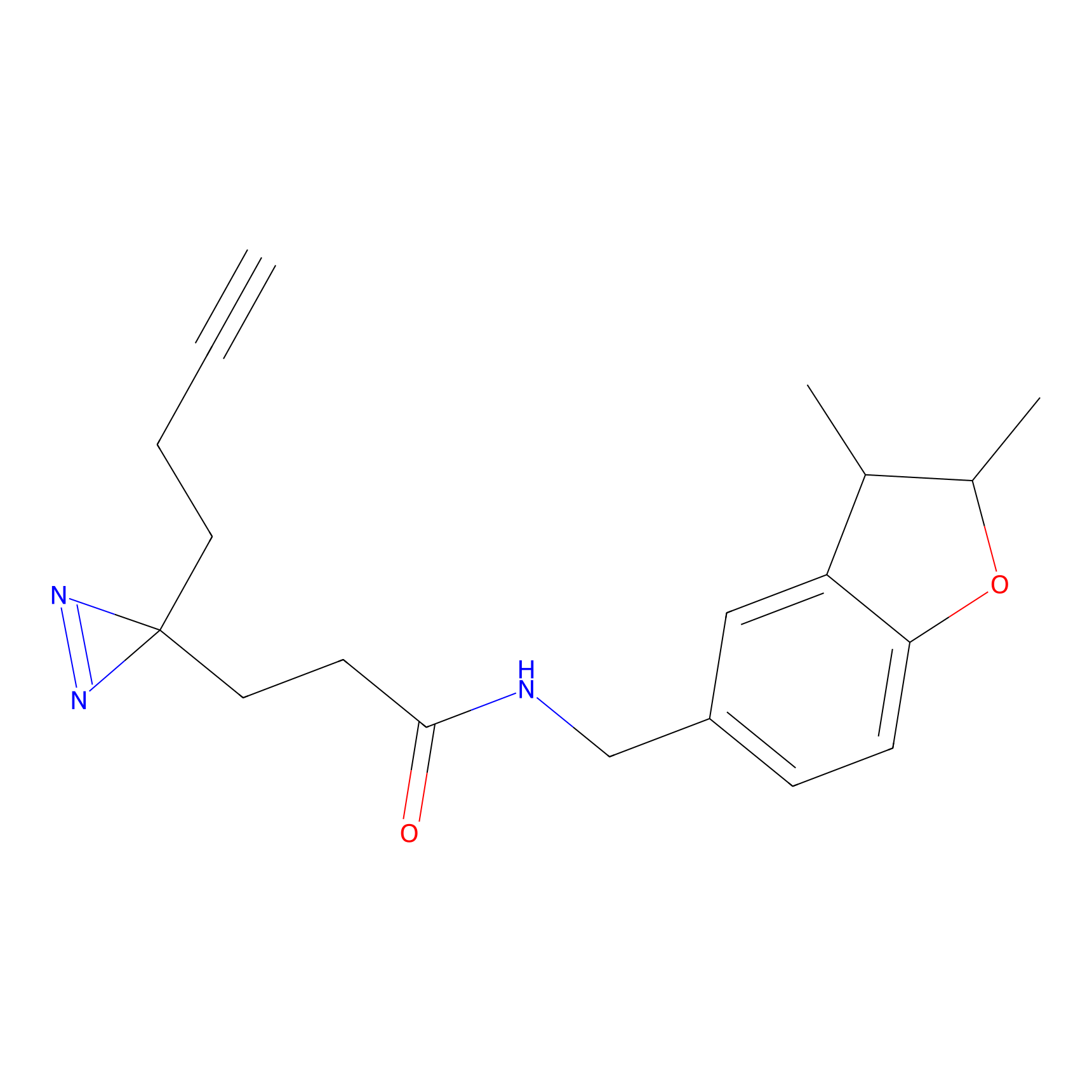
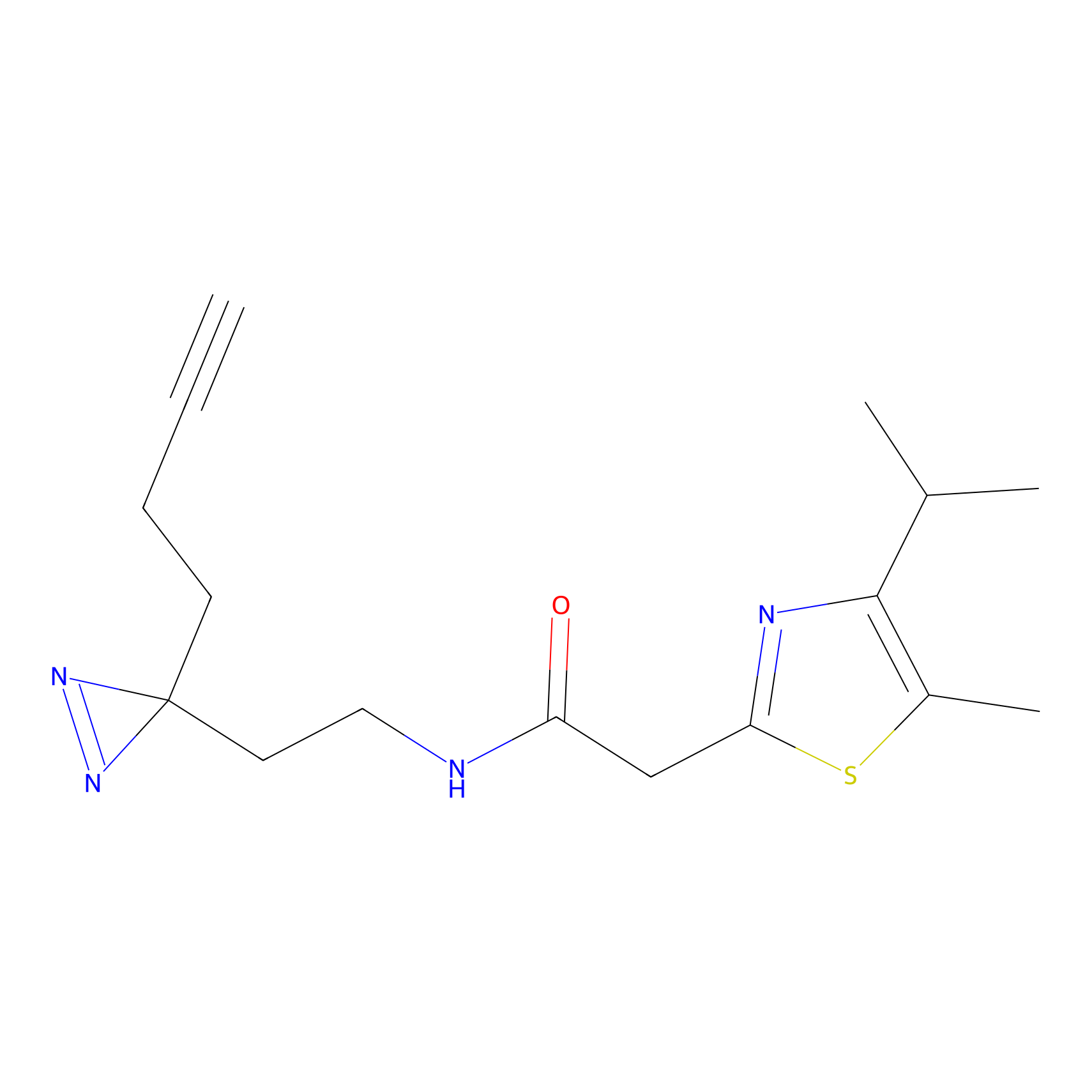
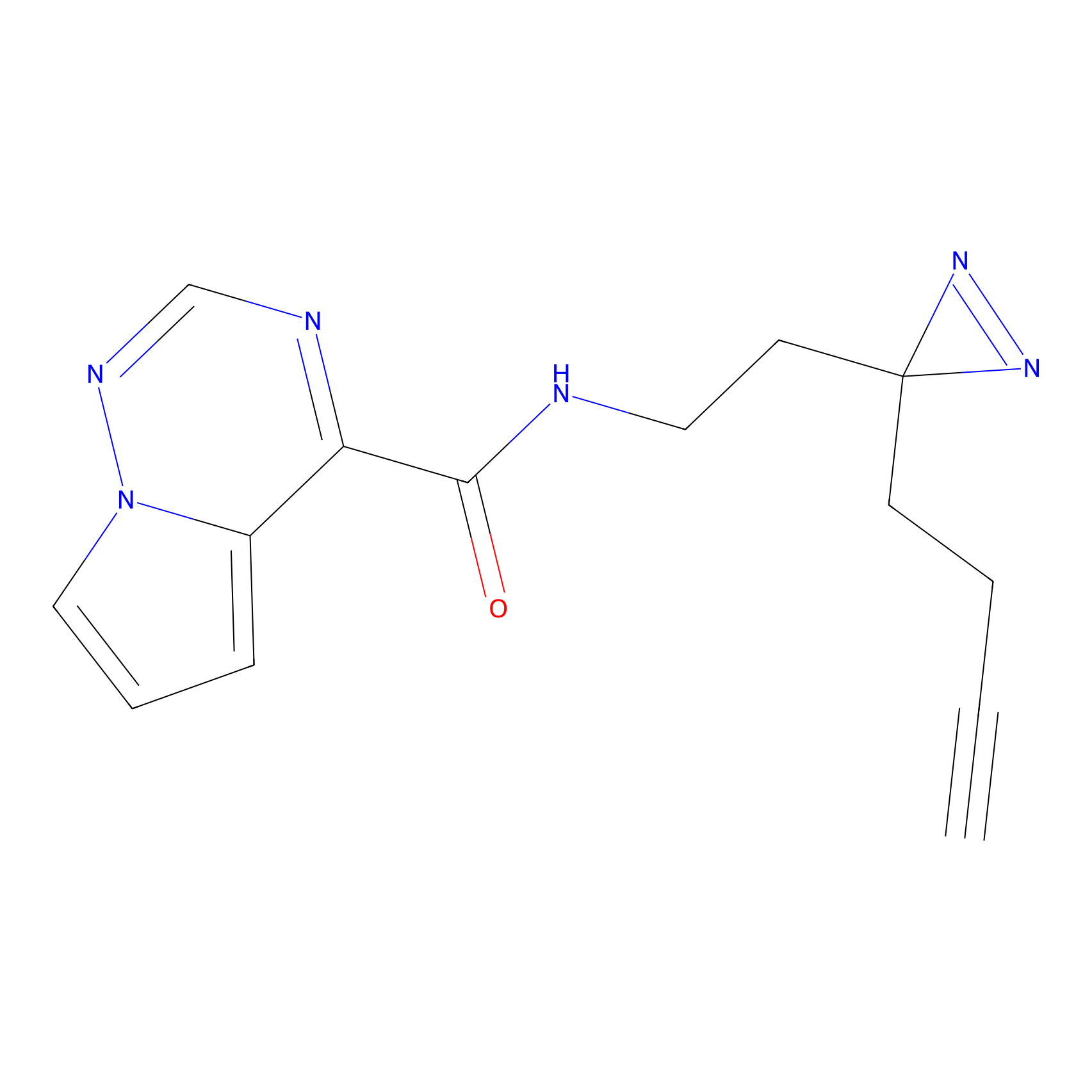
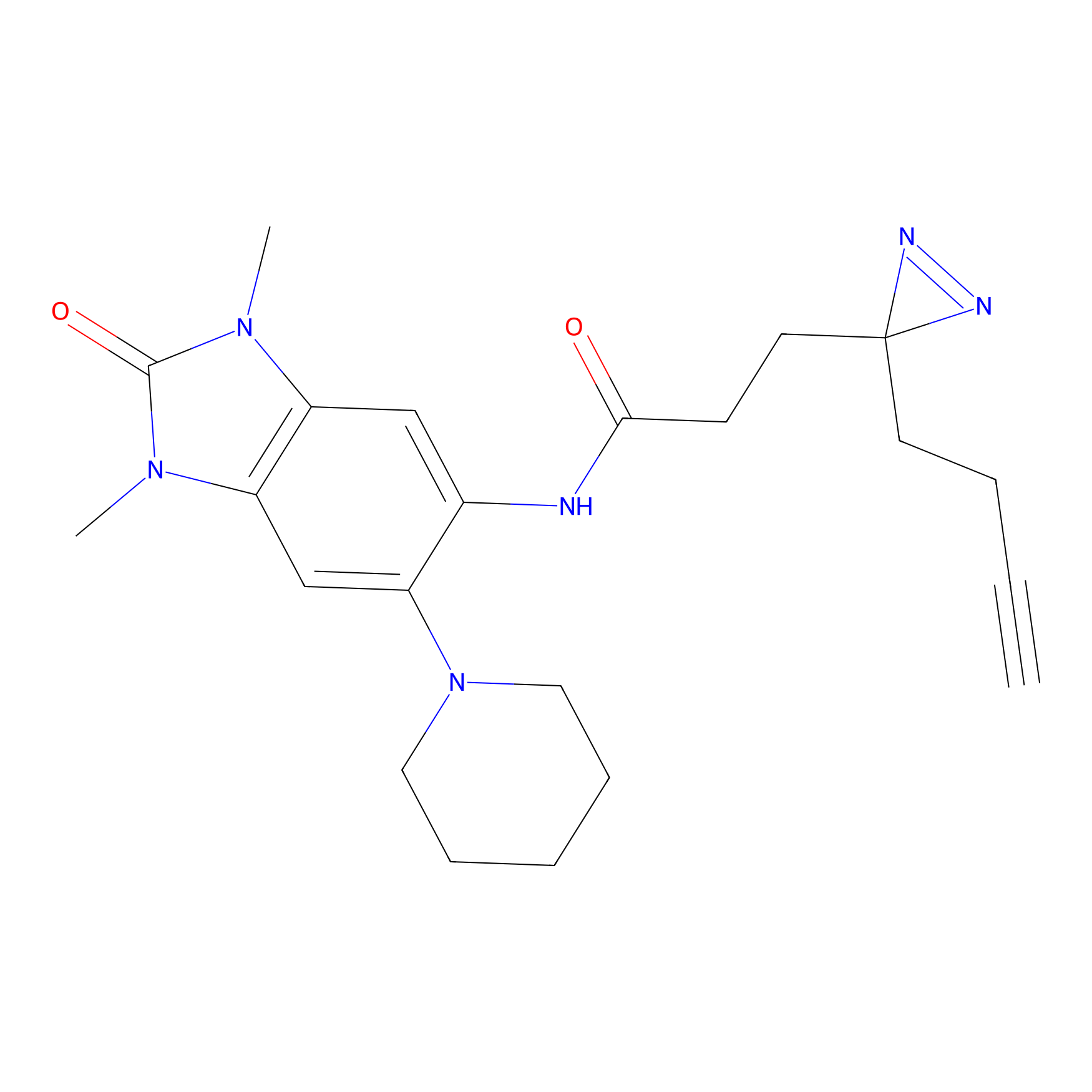
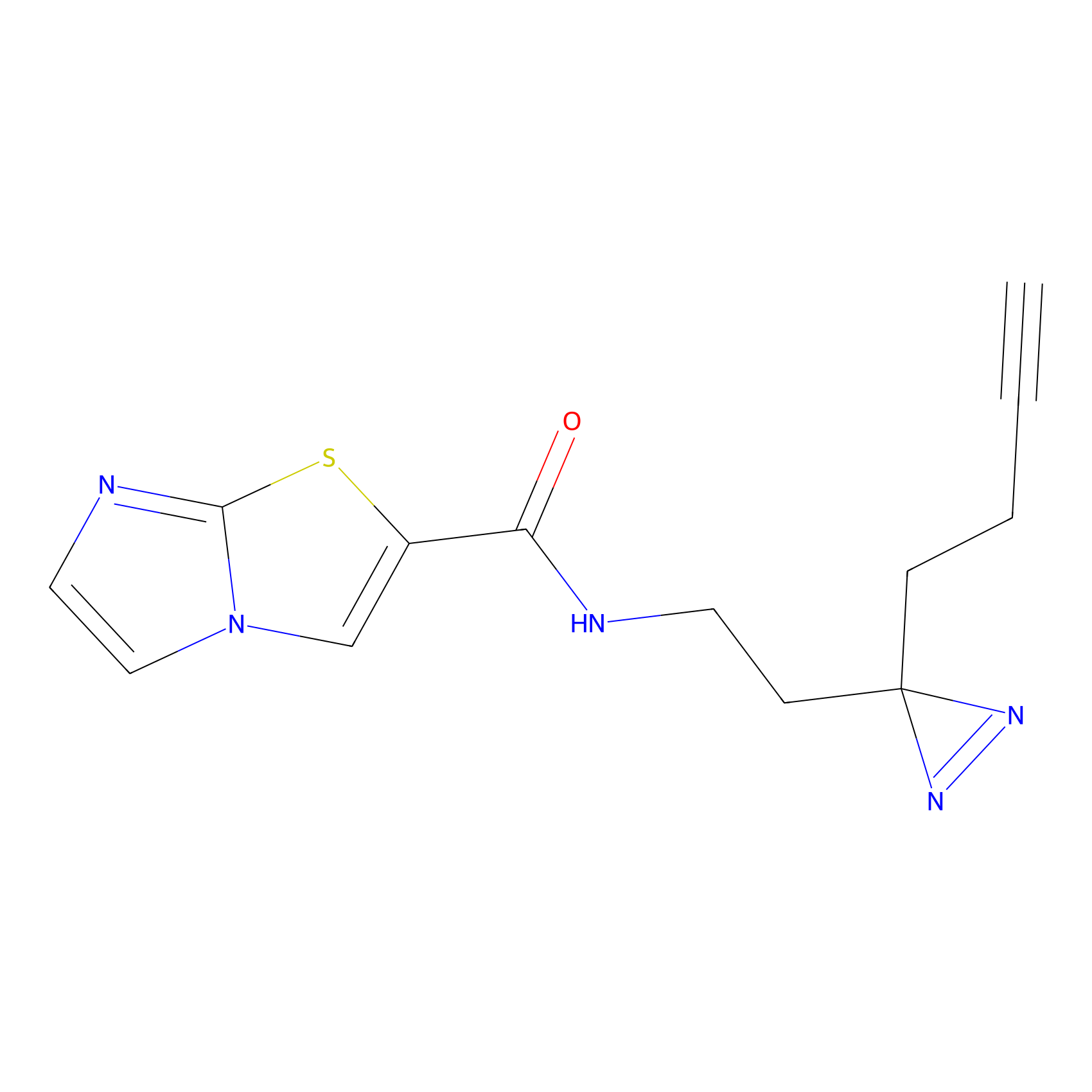
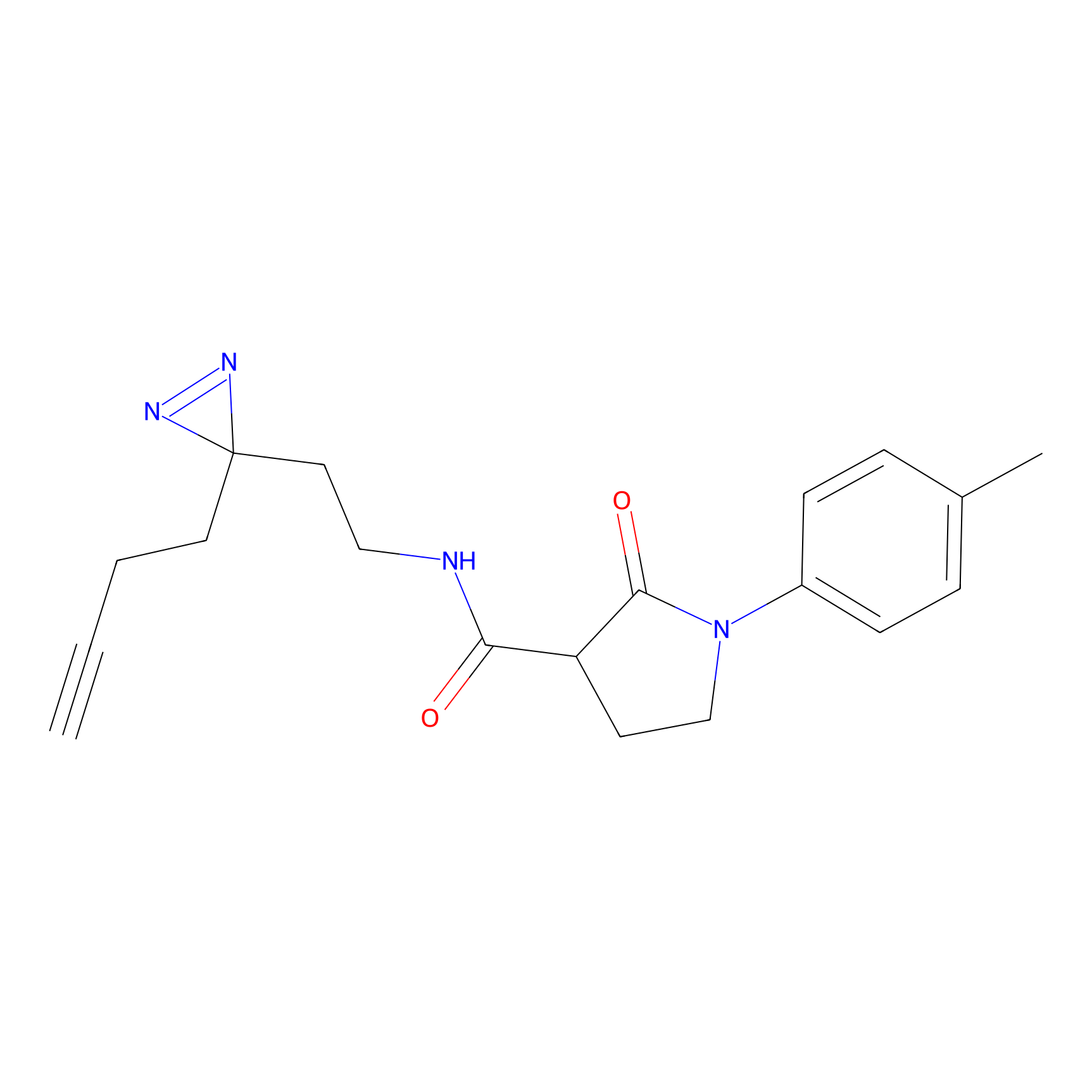
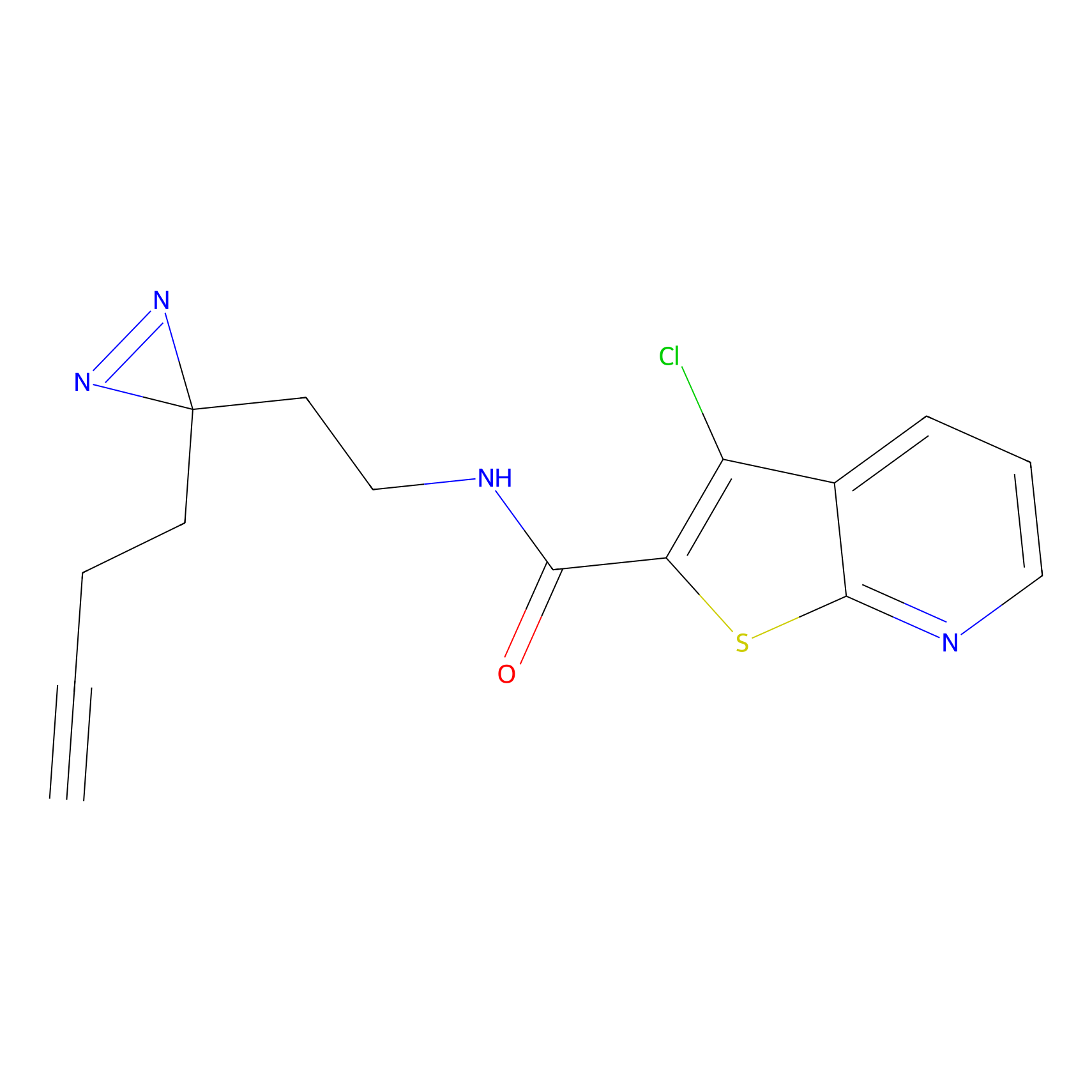
|
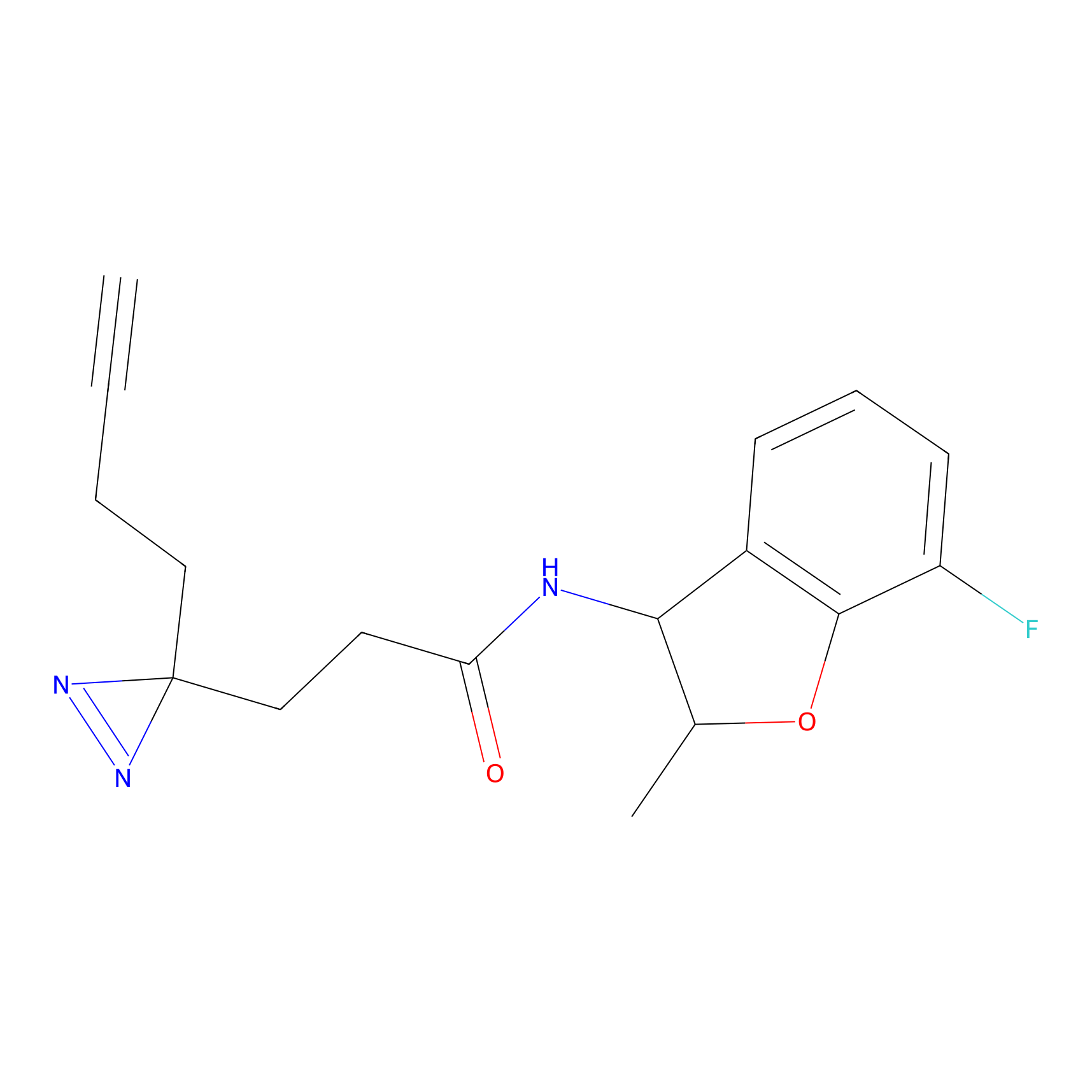
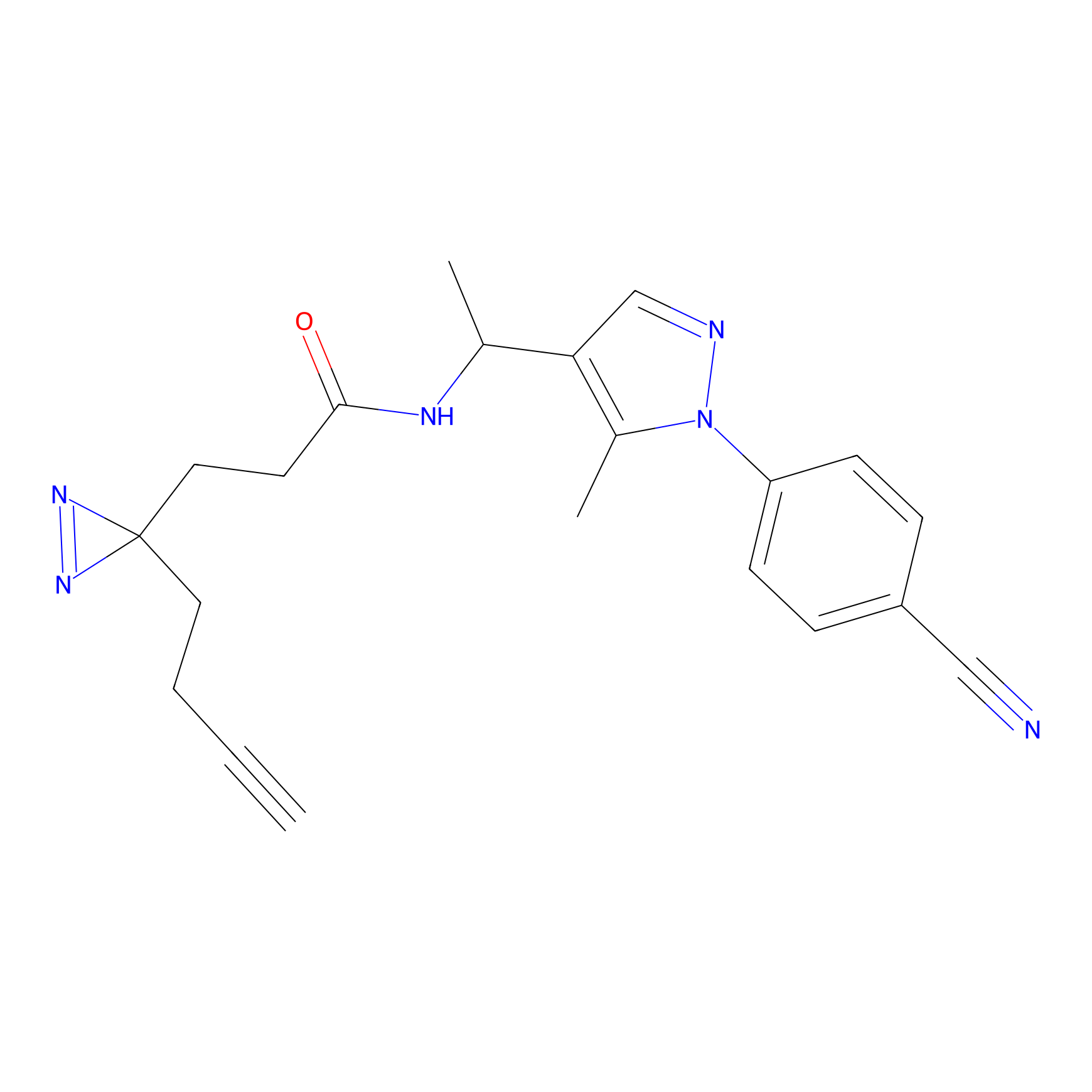
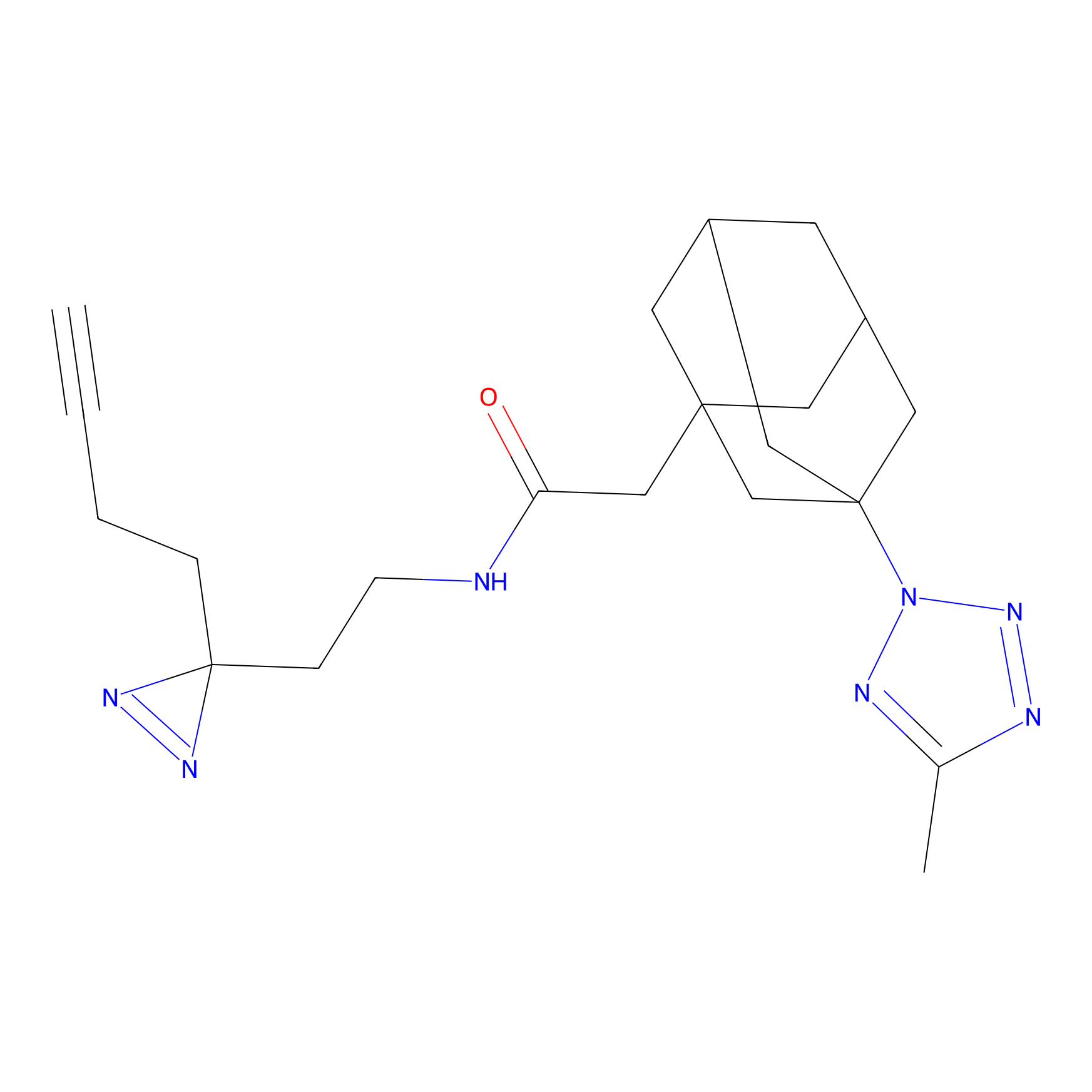
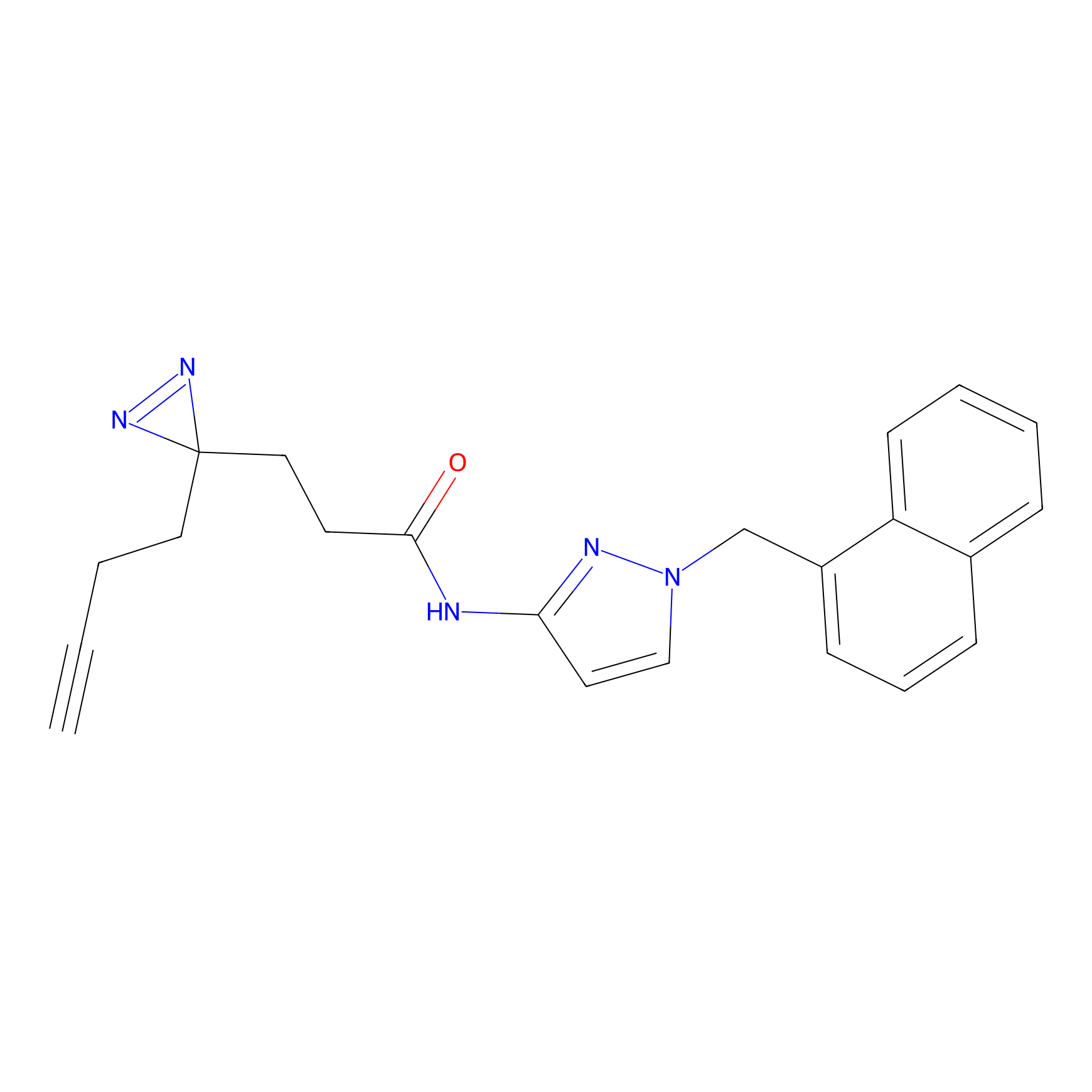
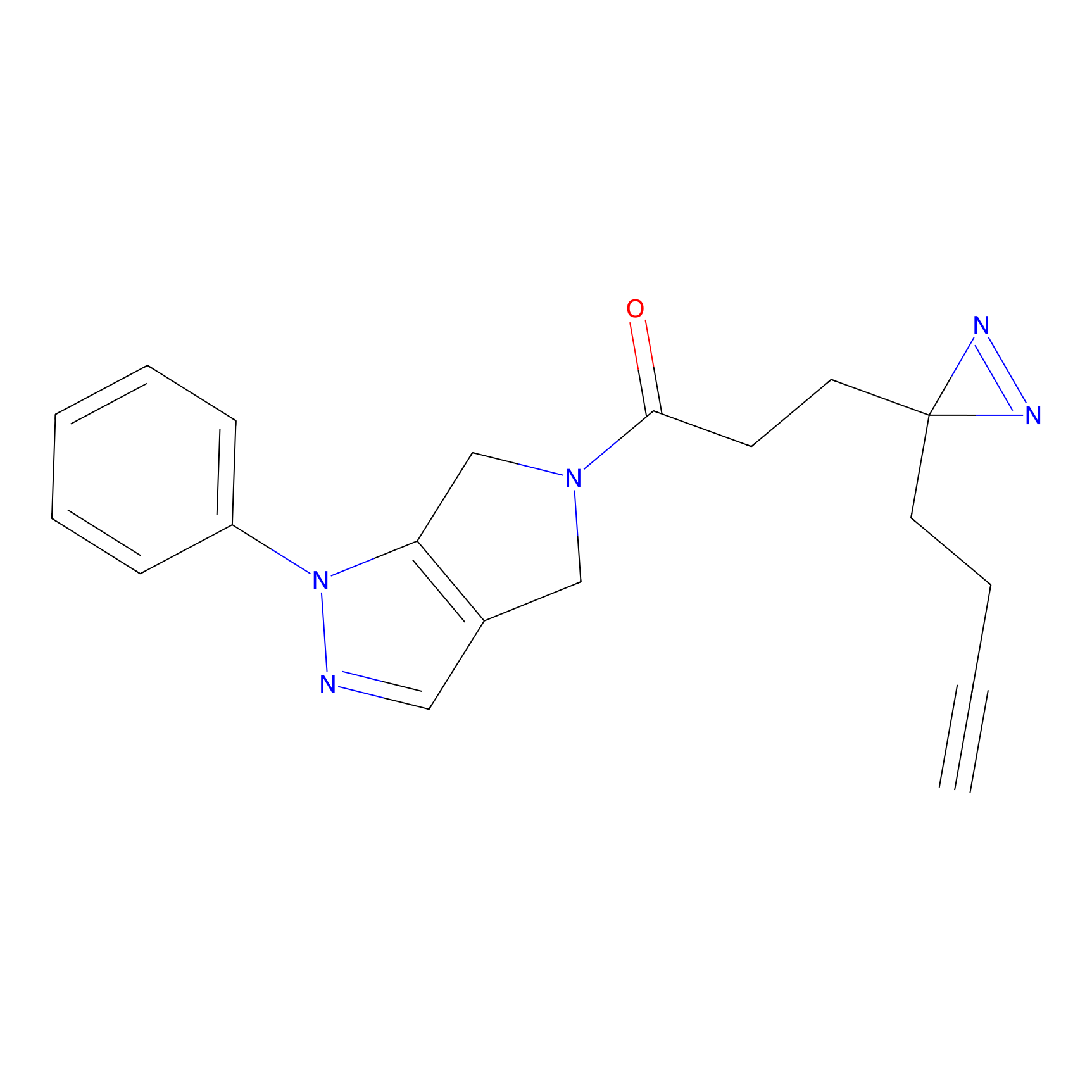
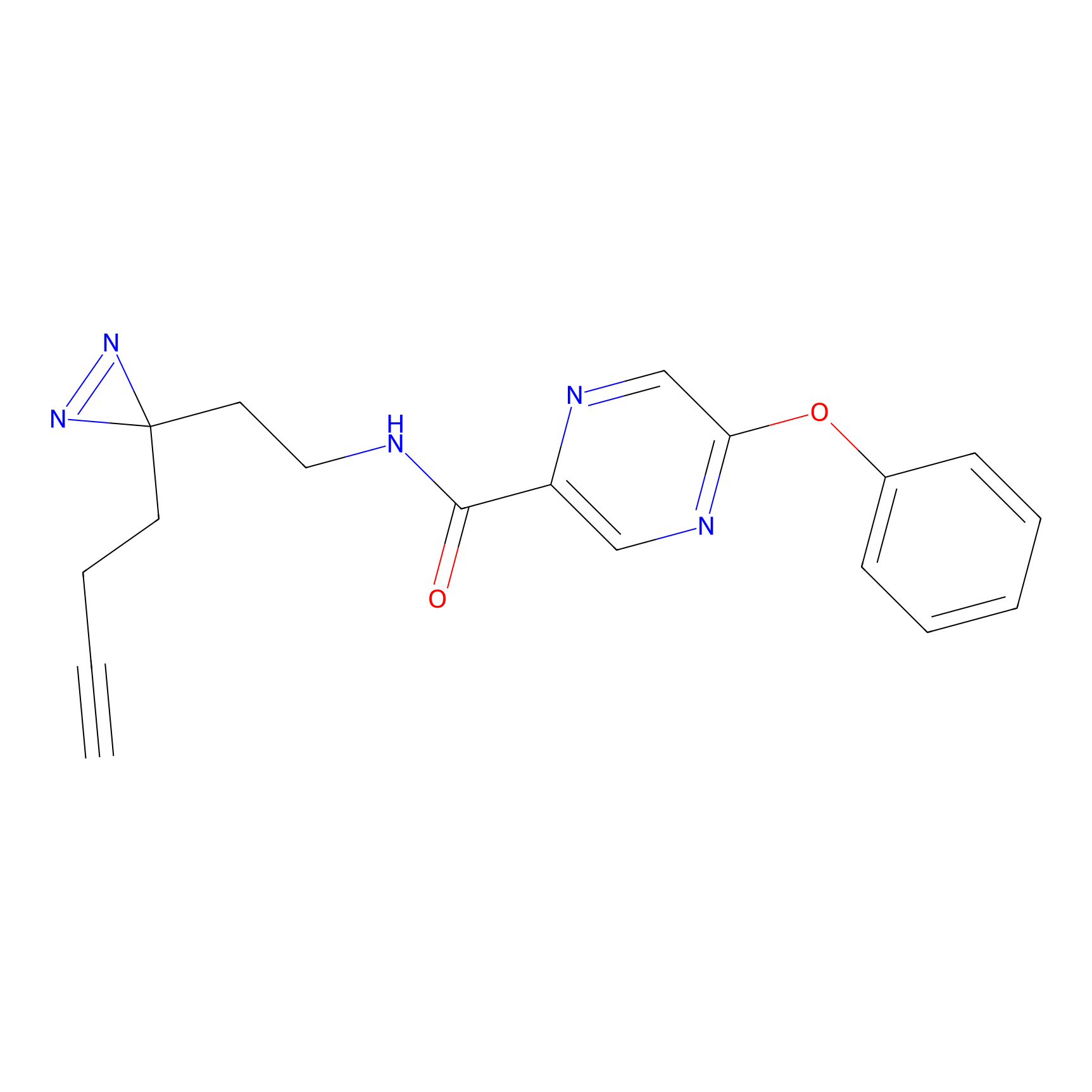
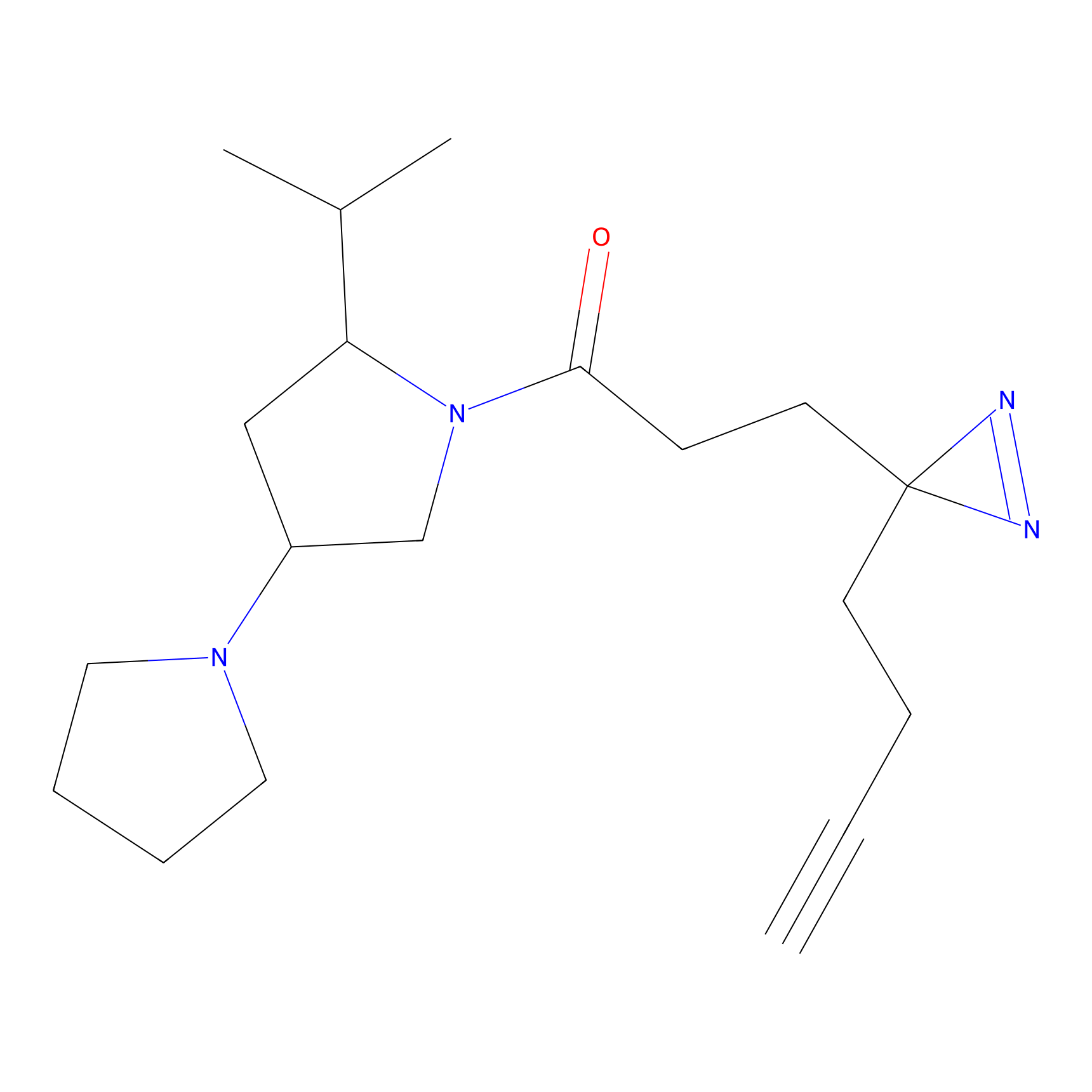
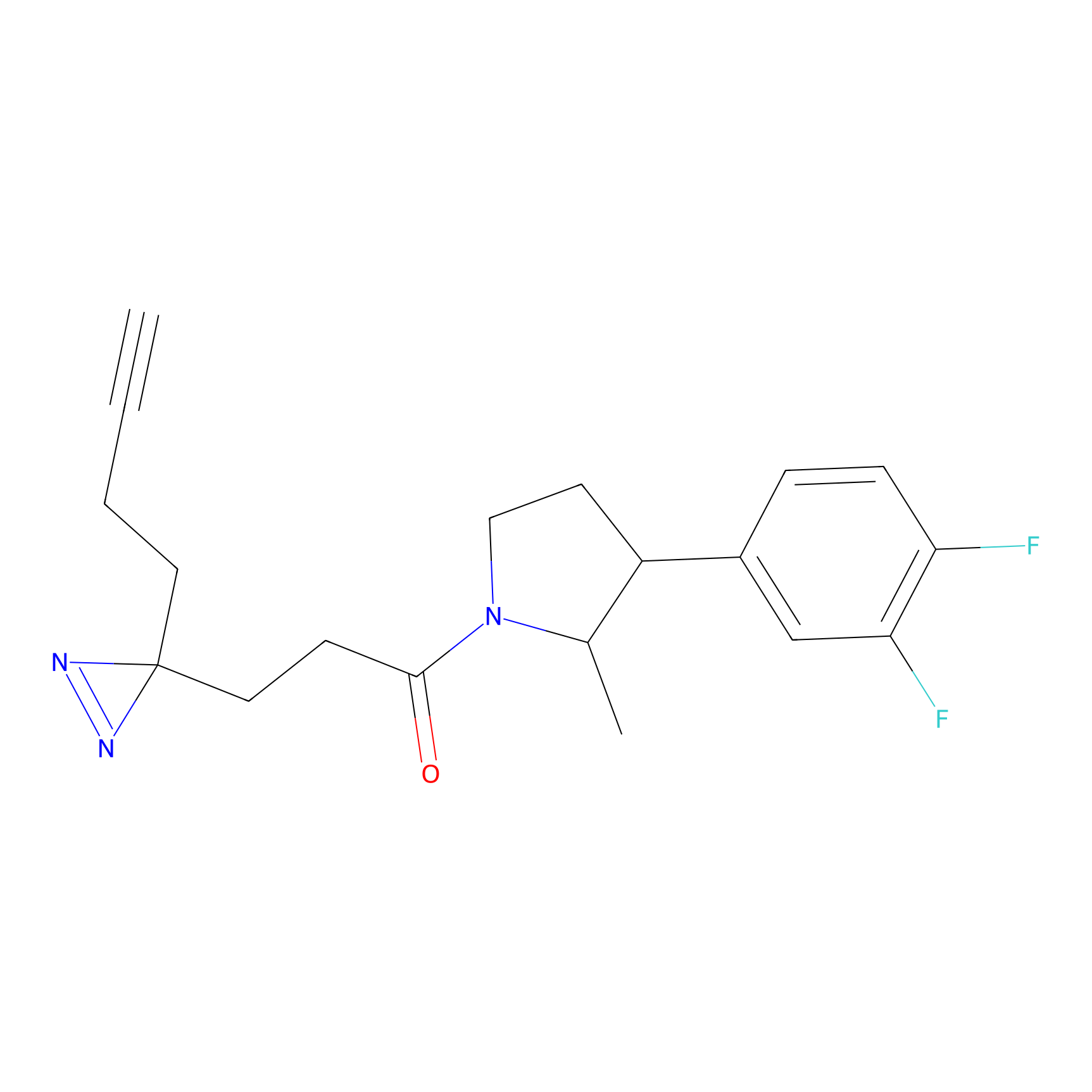
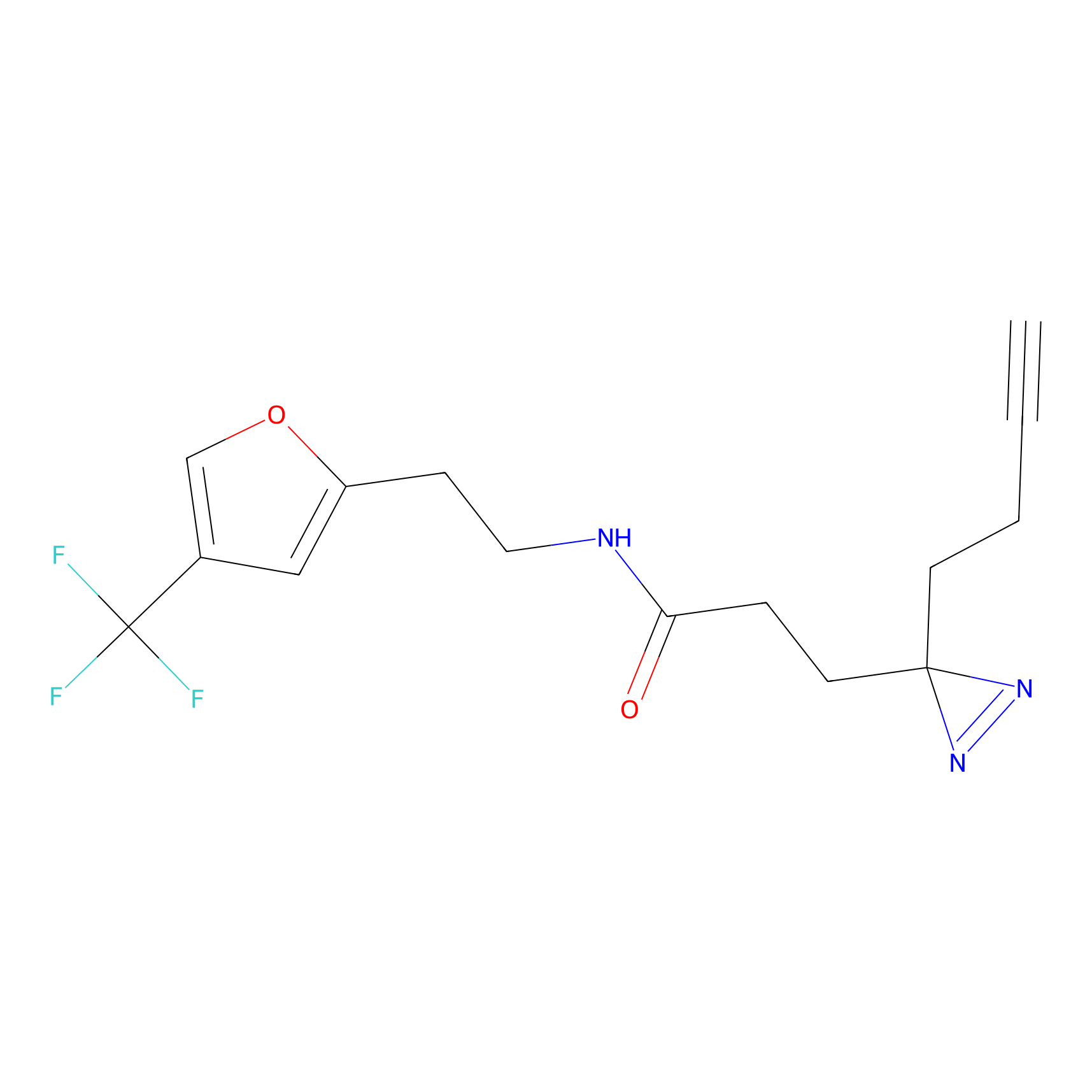
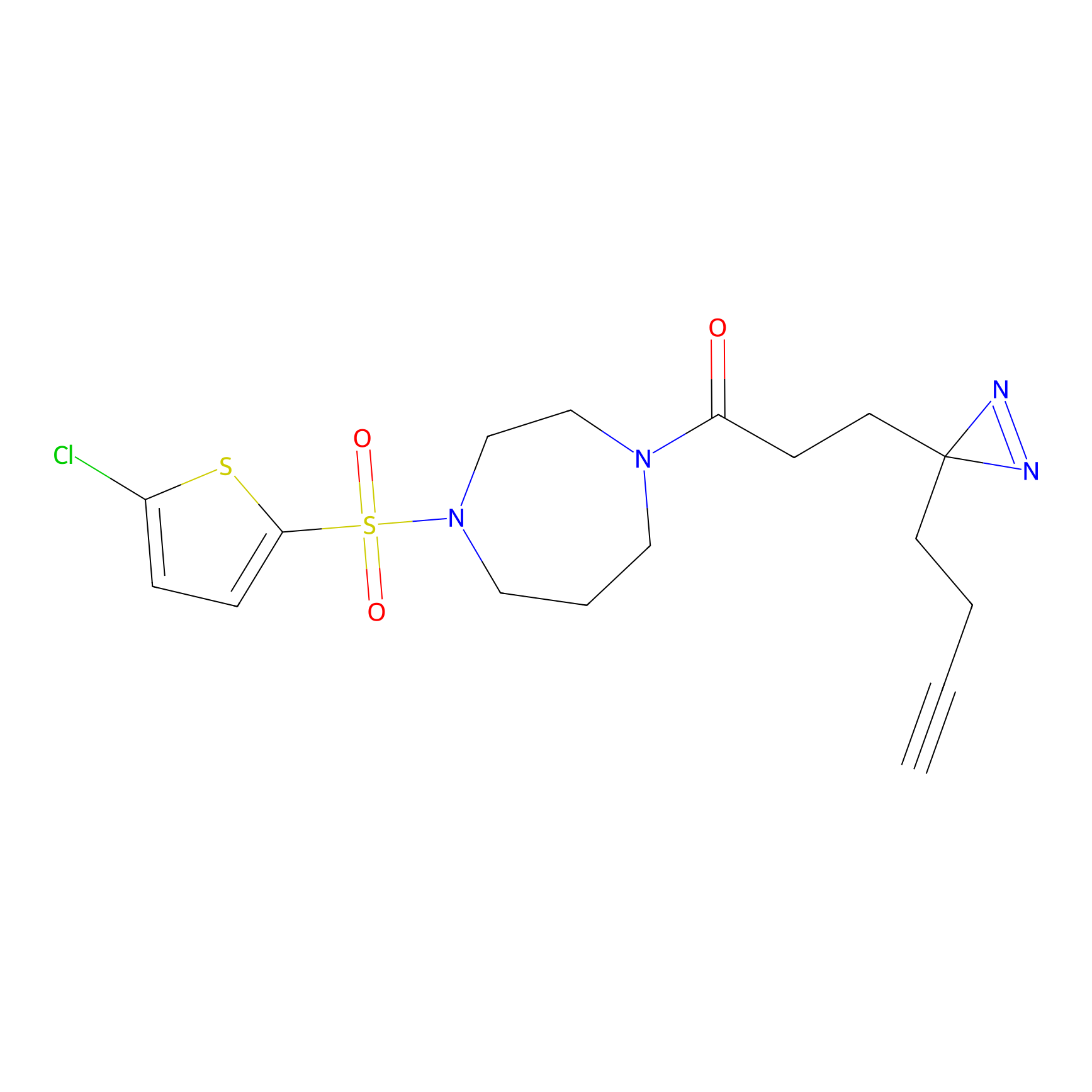
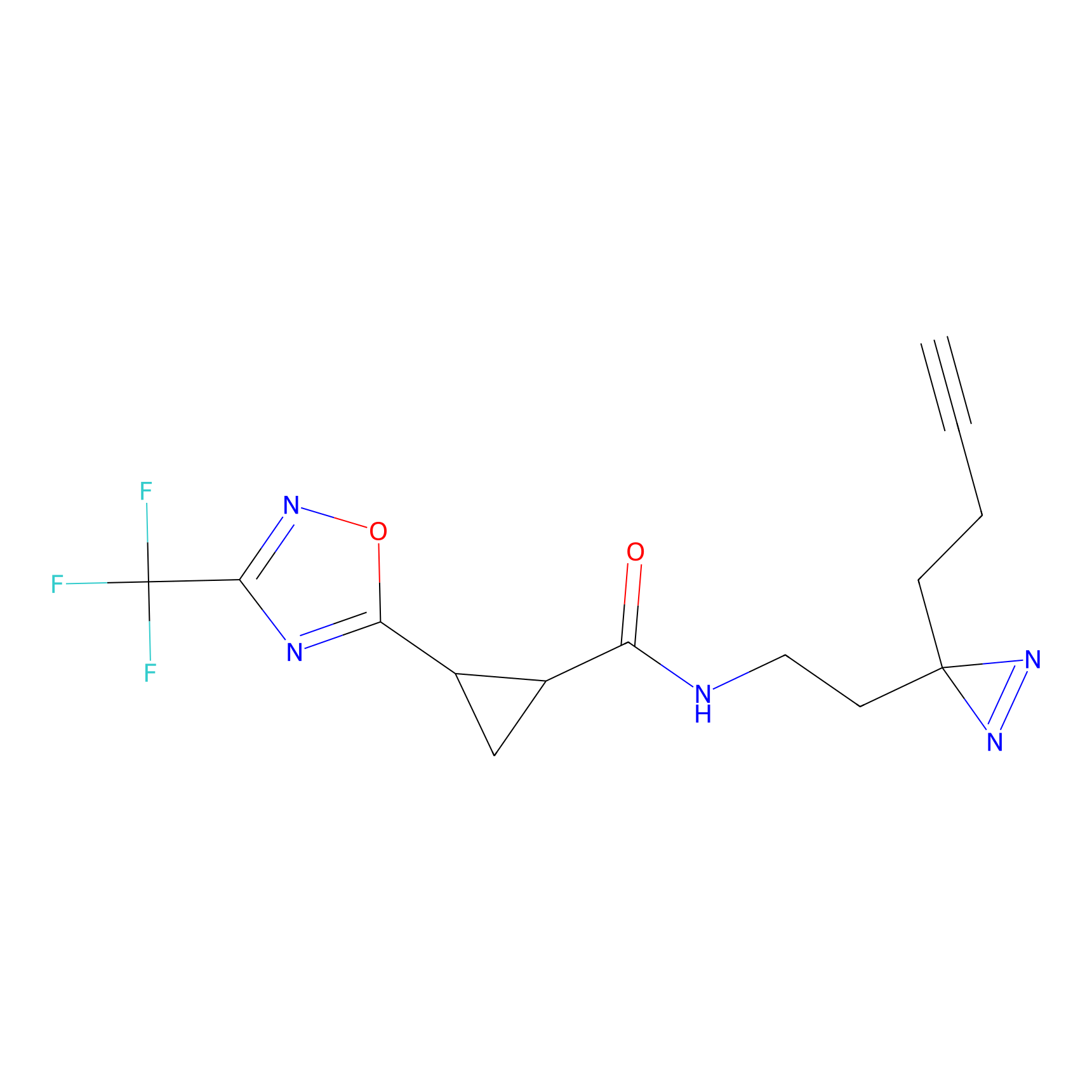
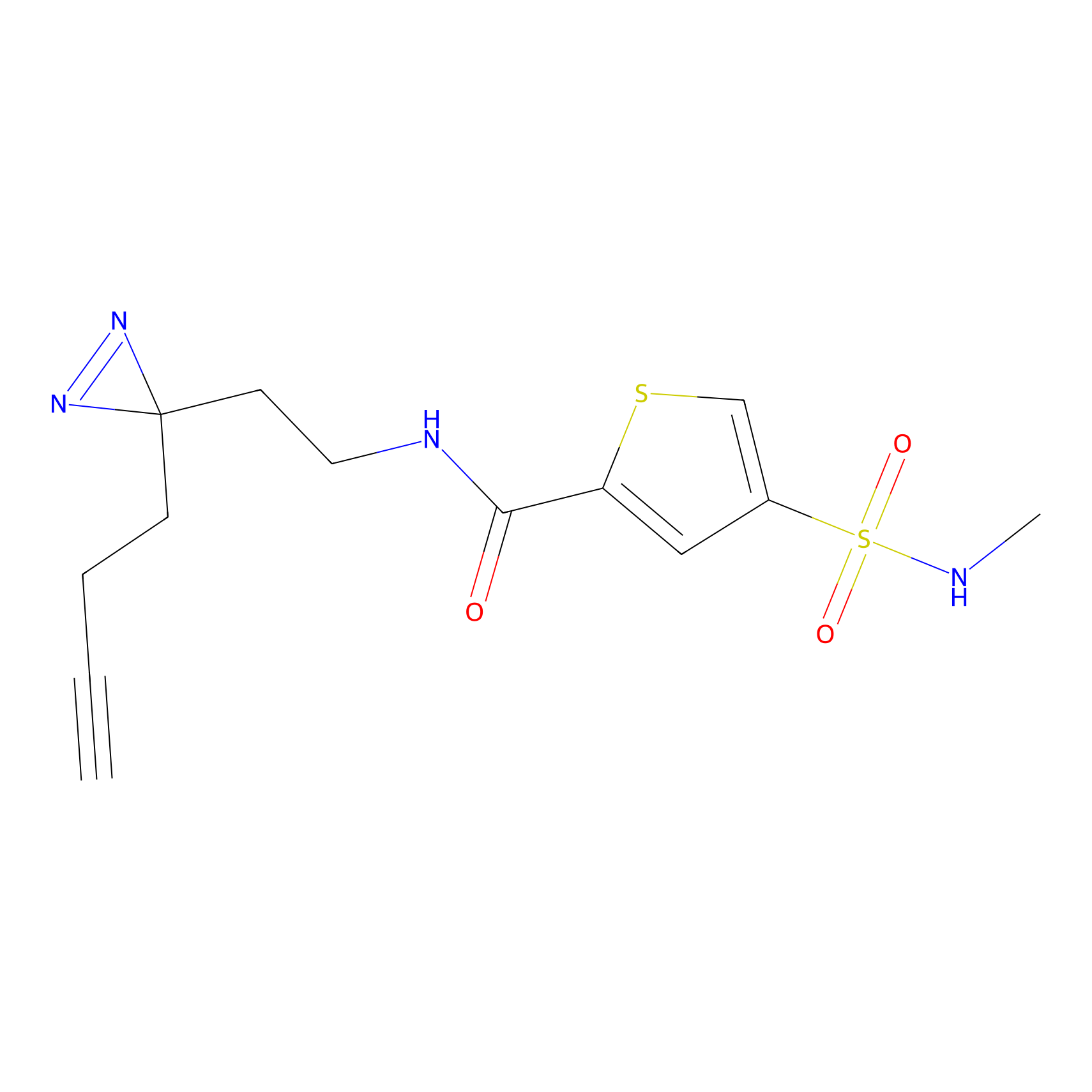
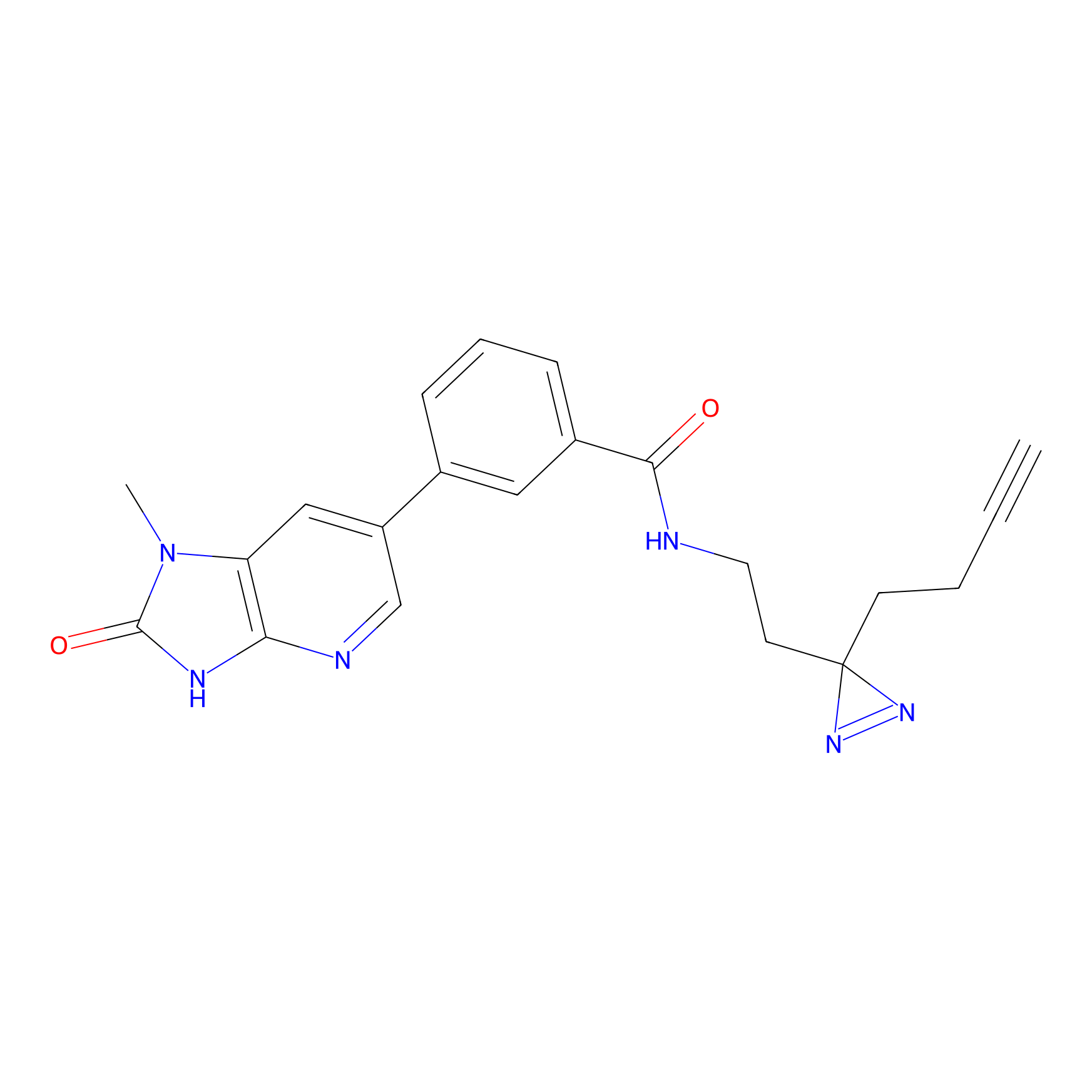
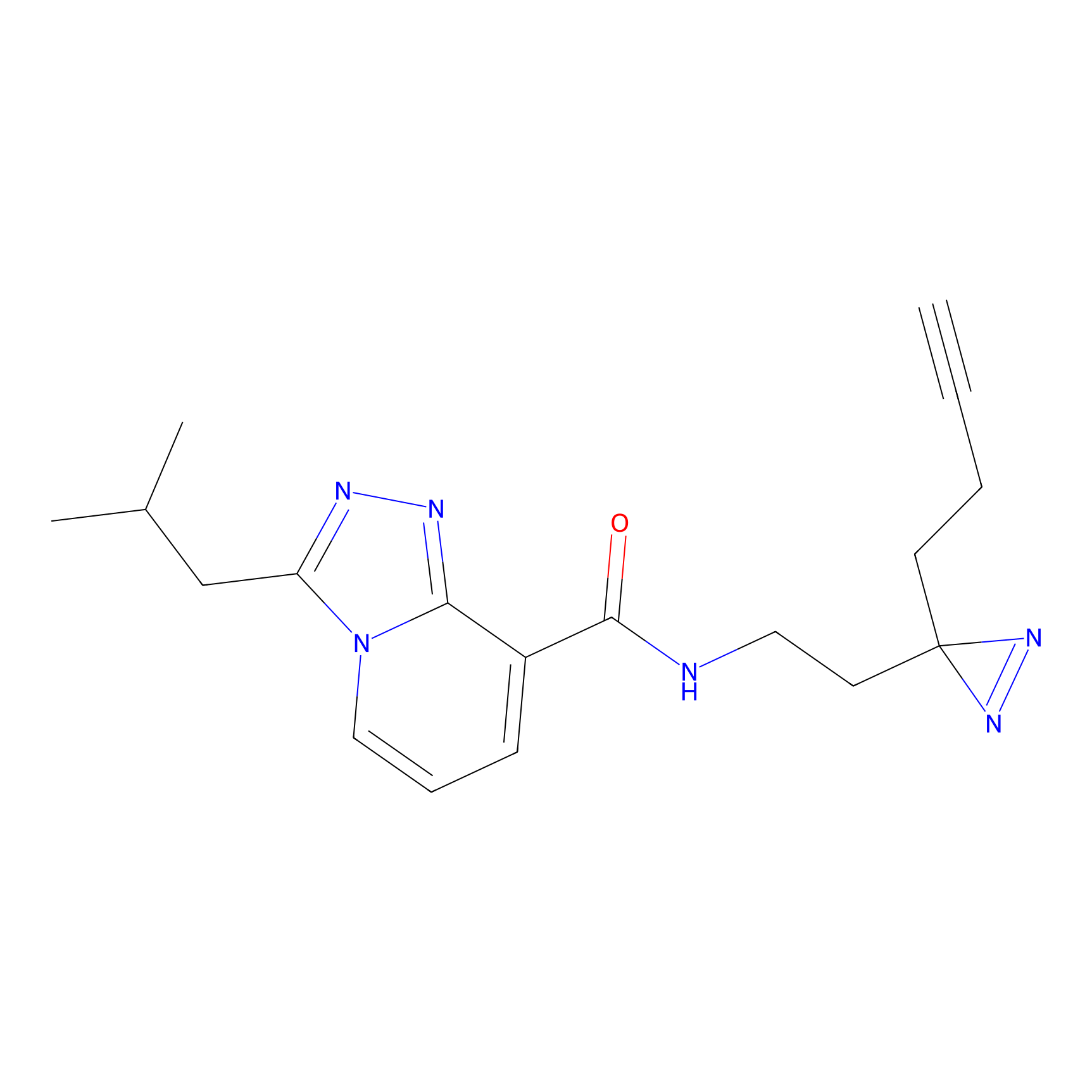
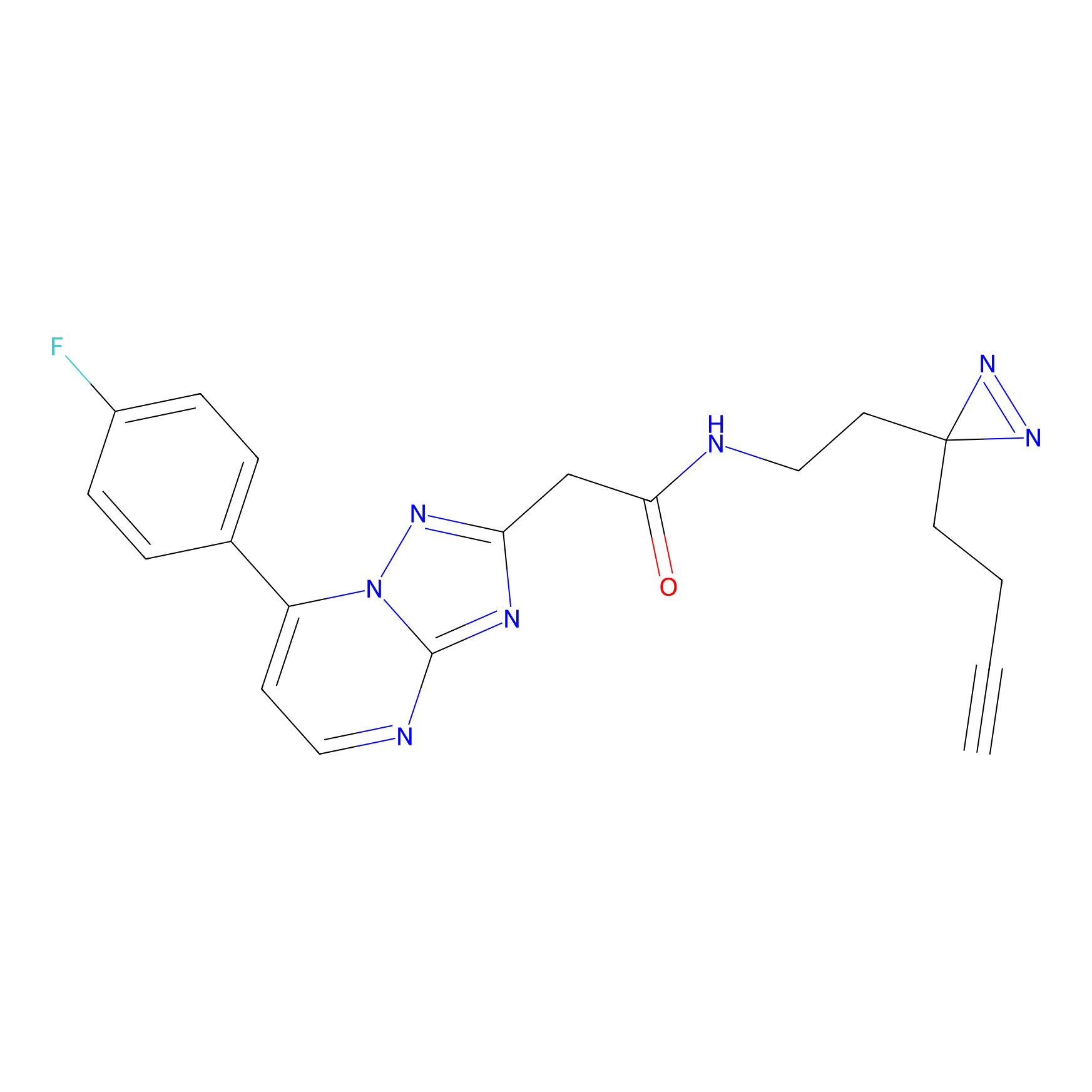
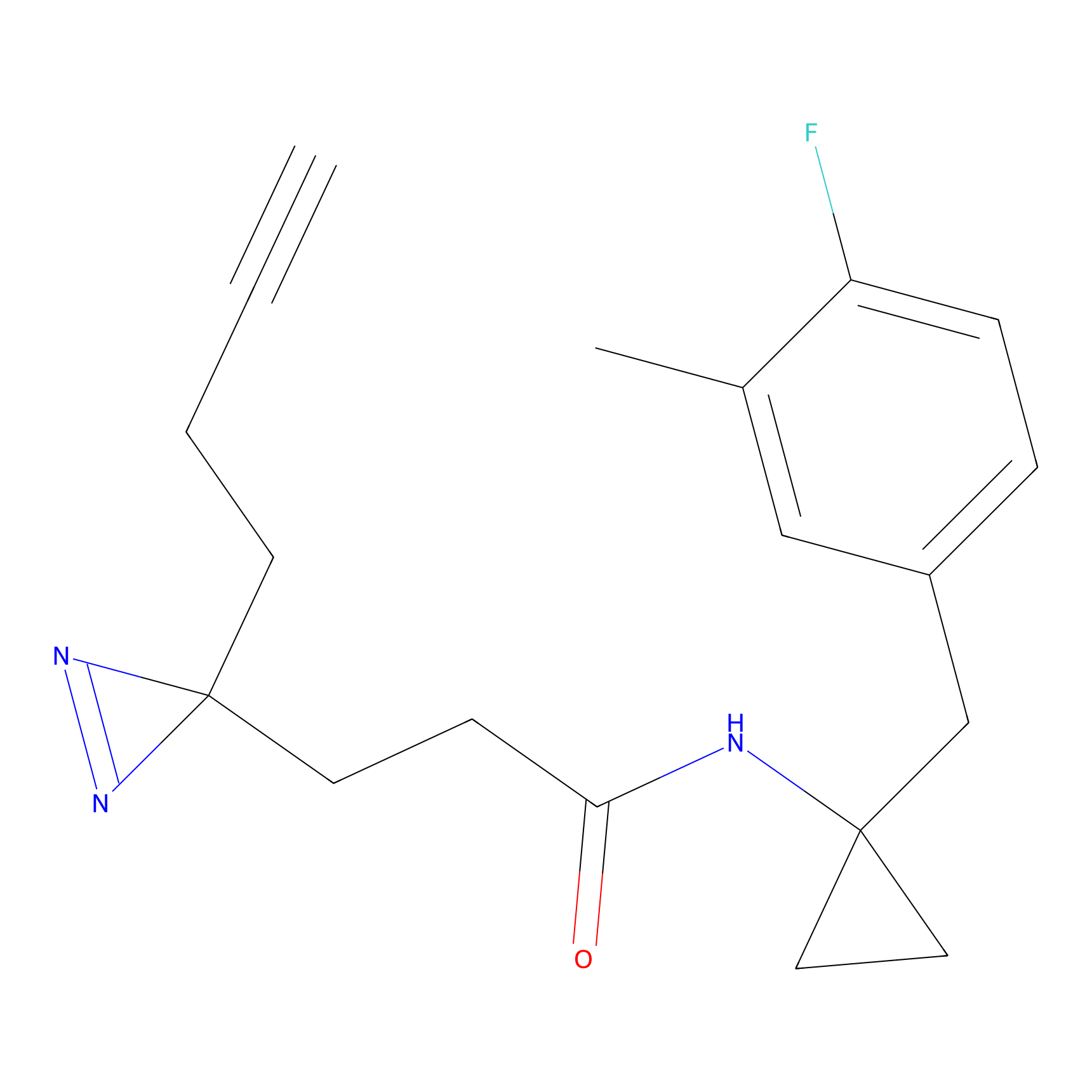
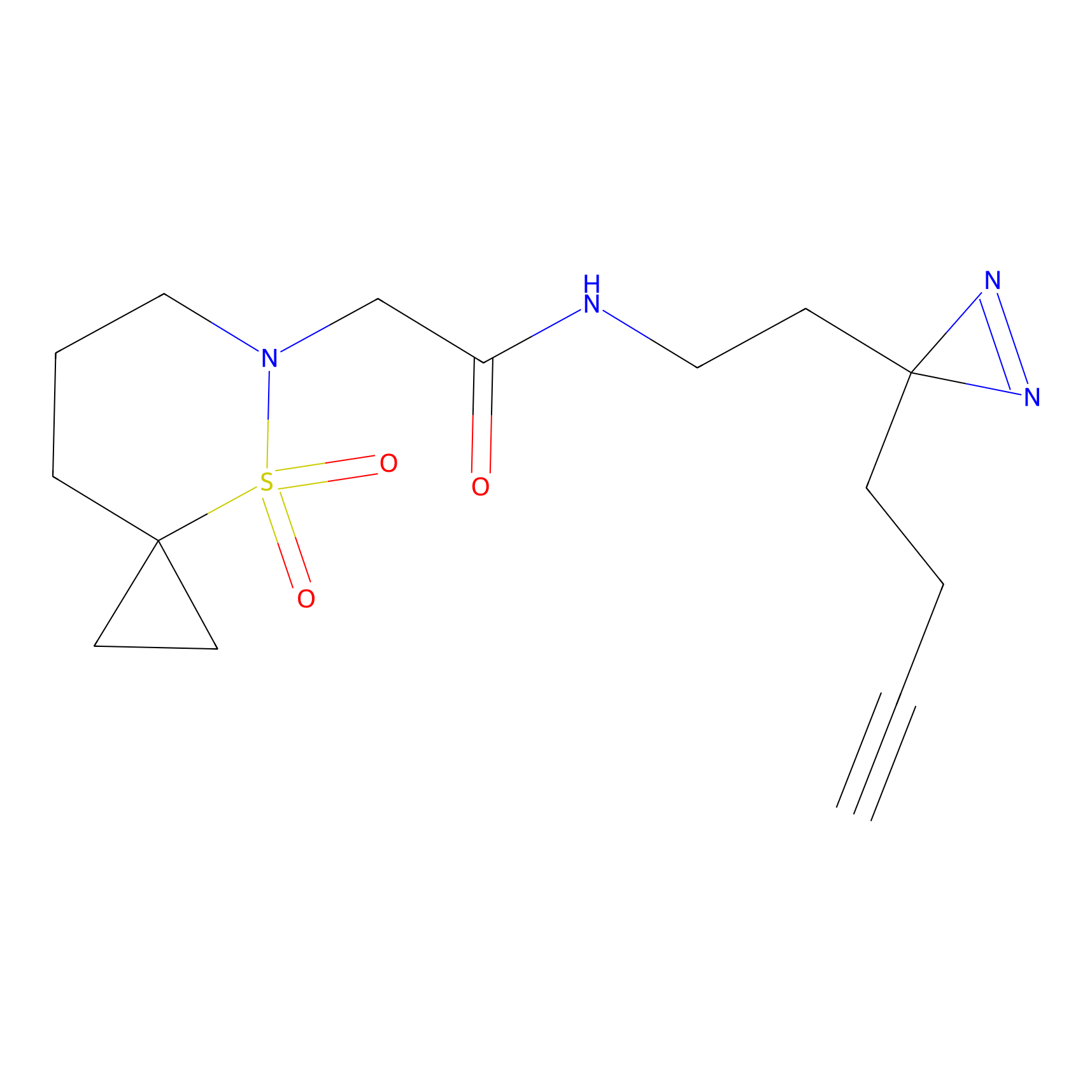
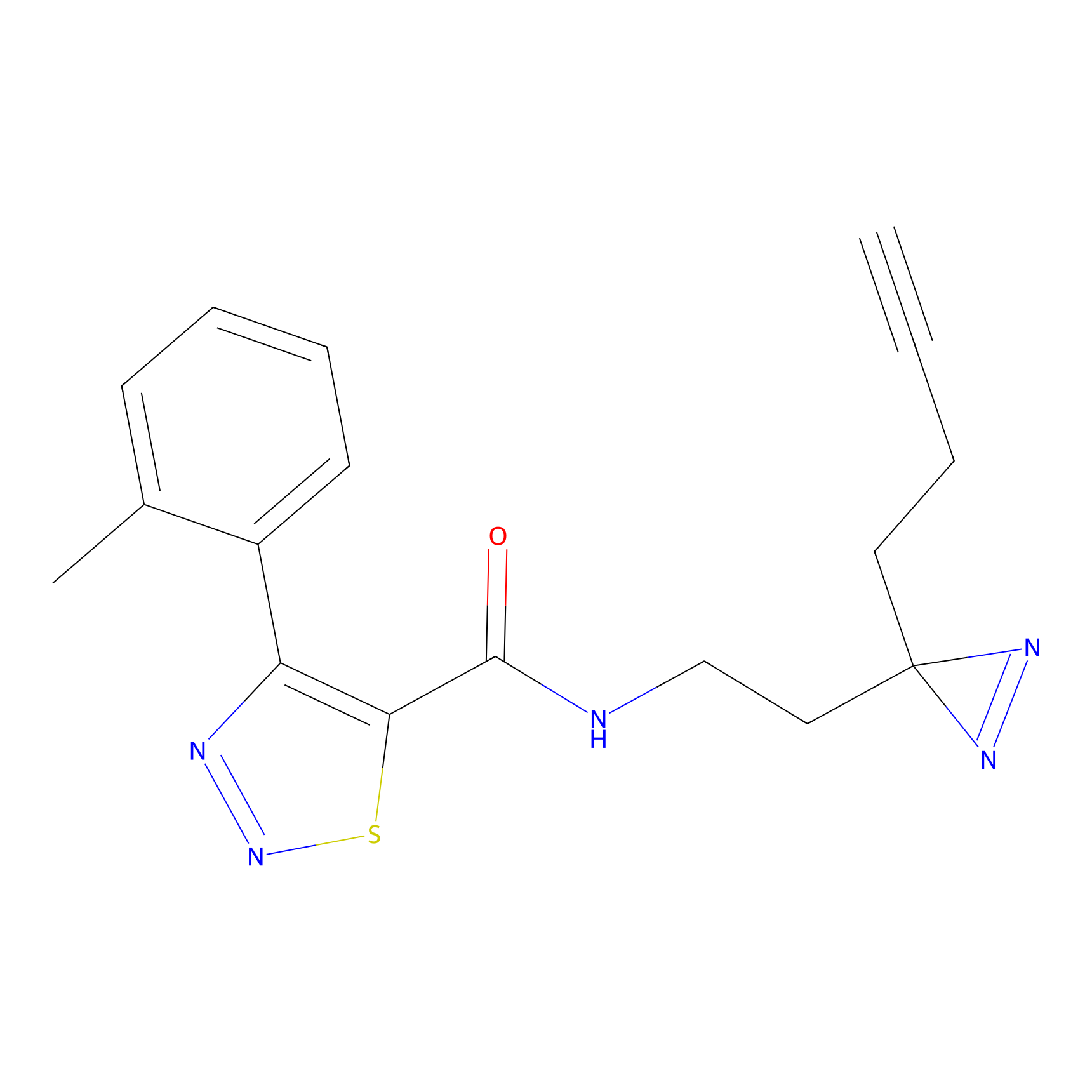
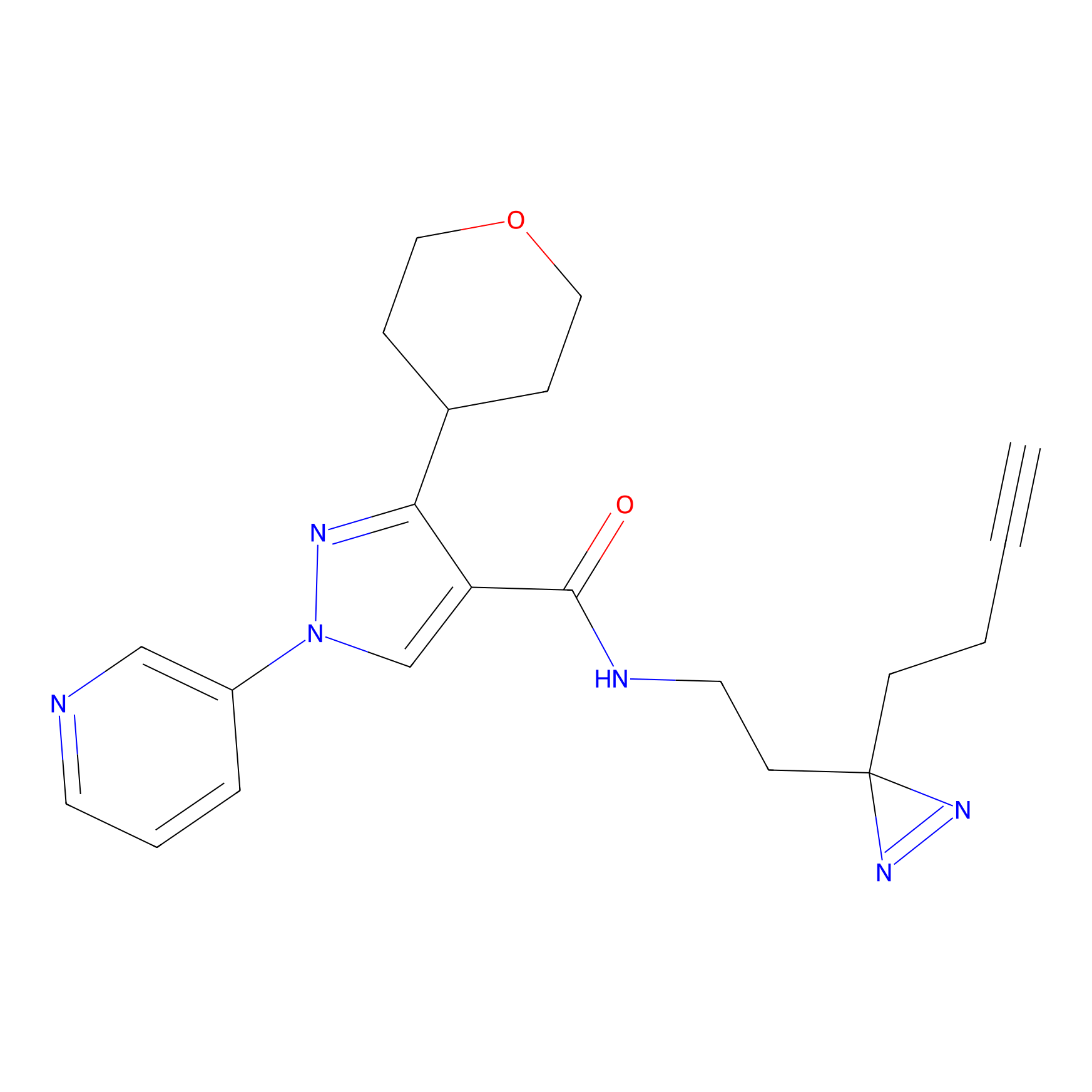
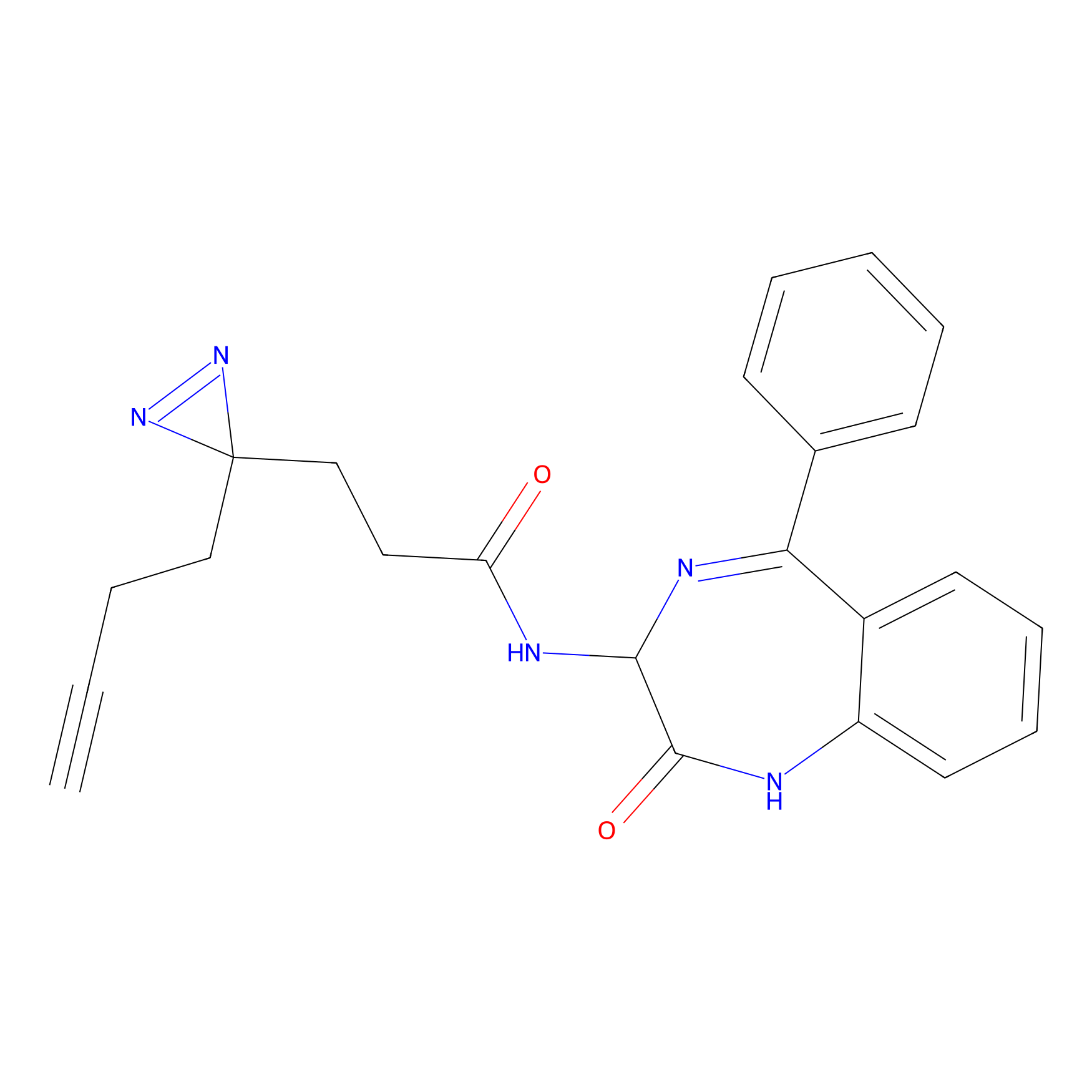
5E-2FA Probe Info |
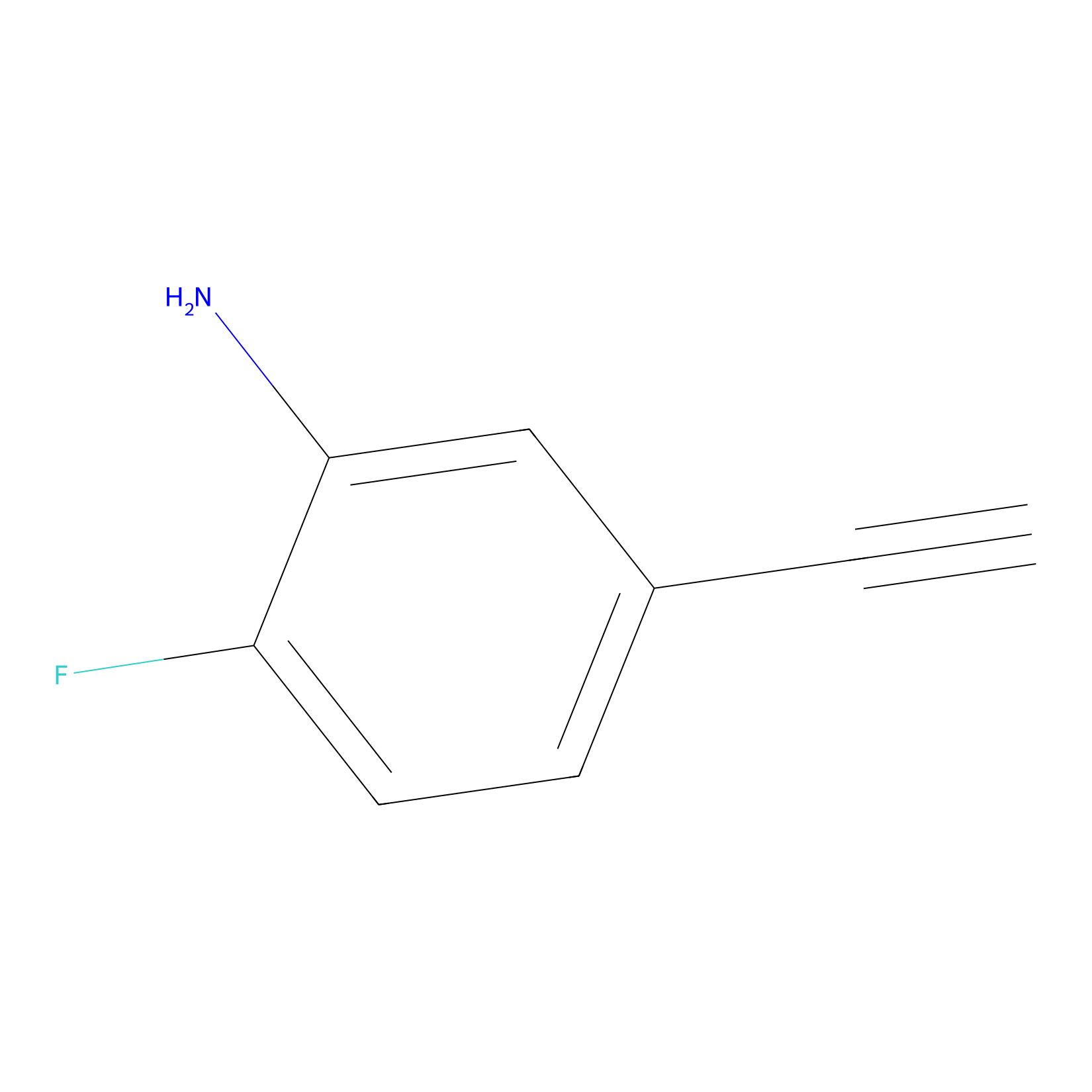 |
N.A. | LDD2235 | [3] | |
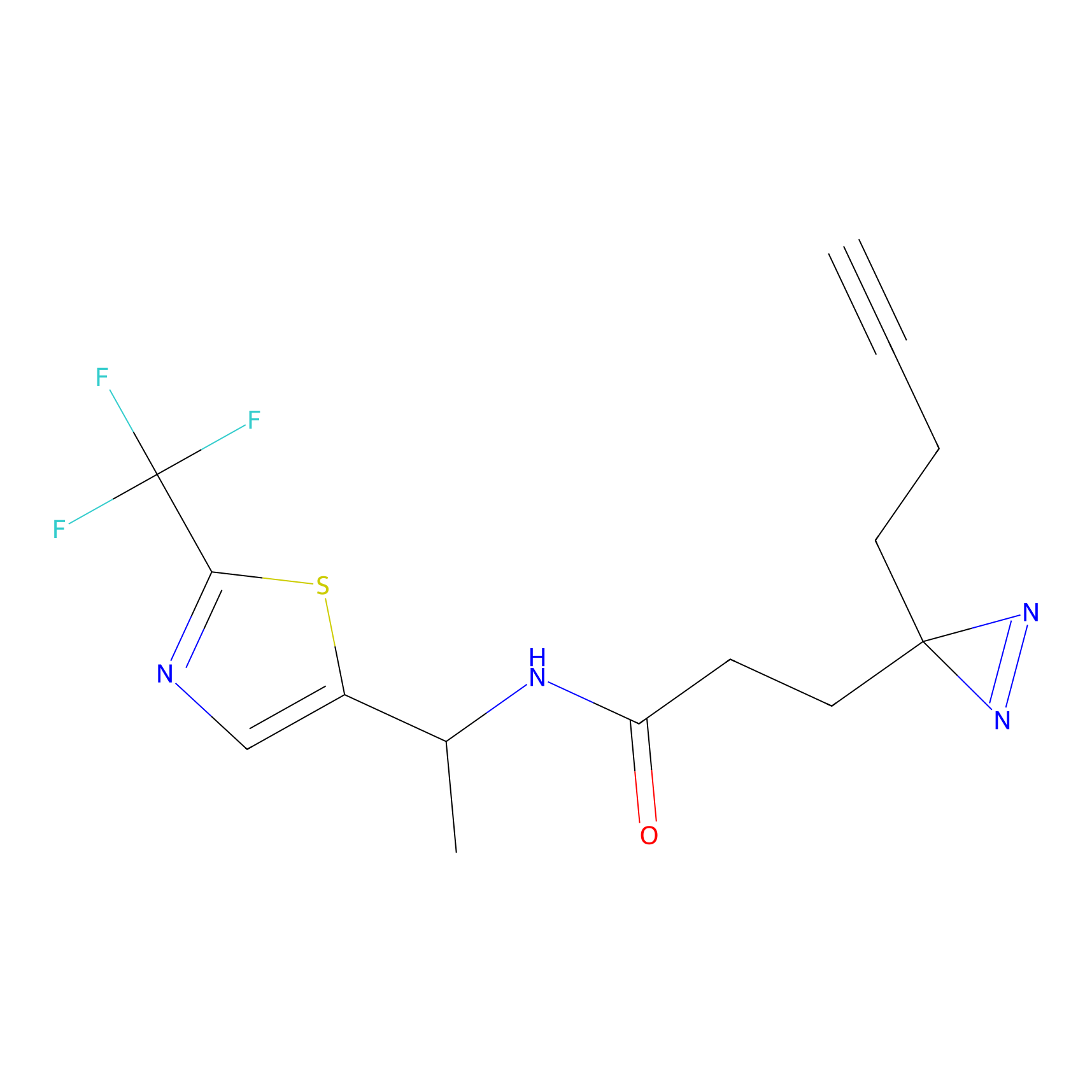
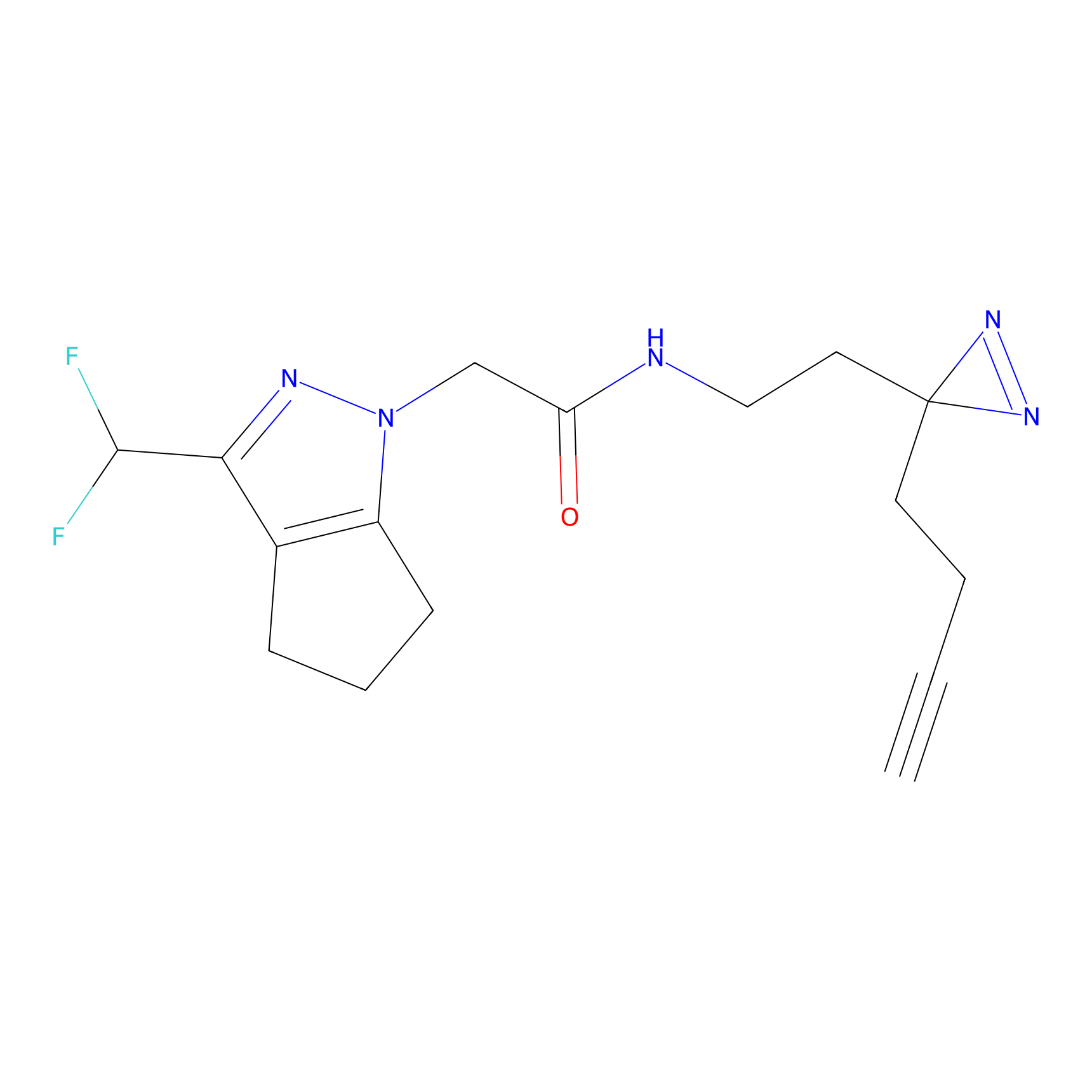
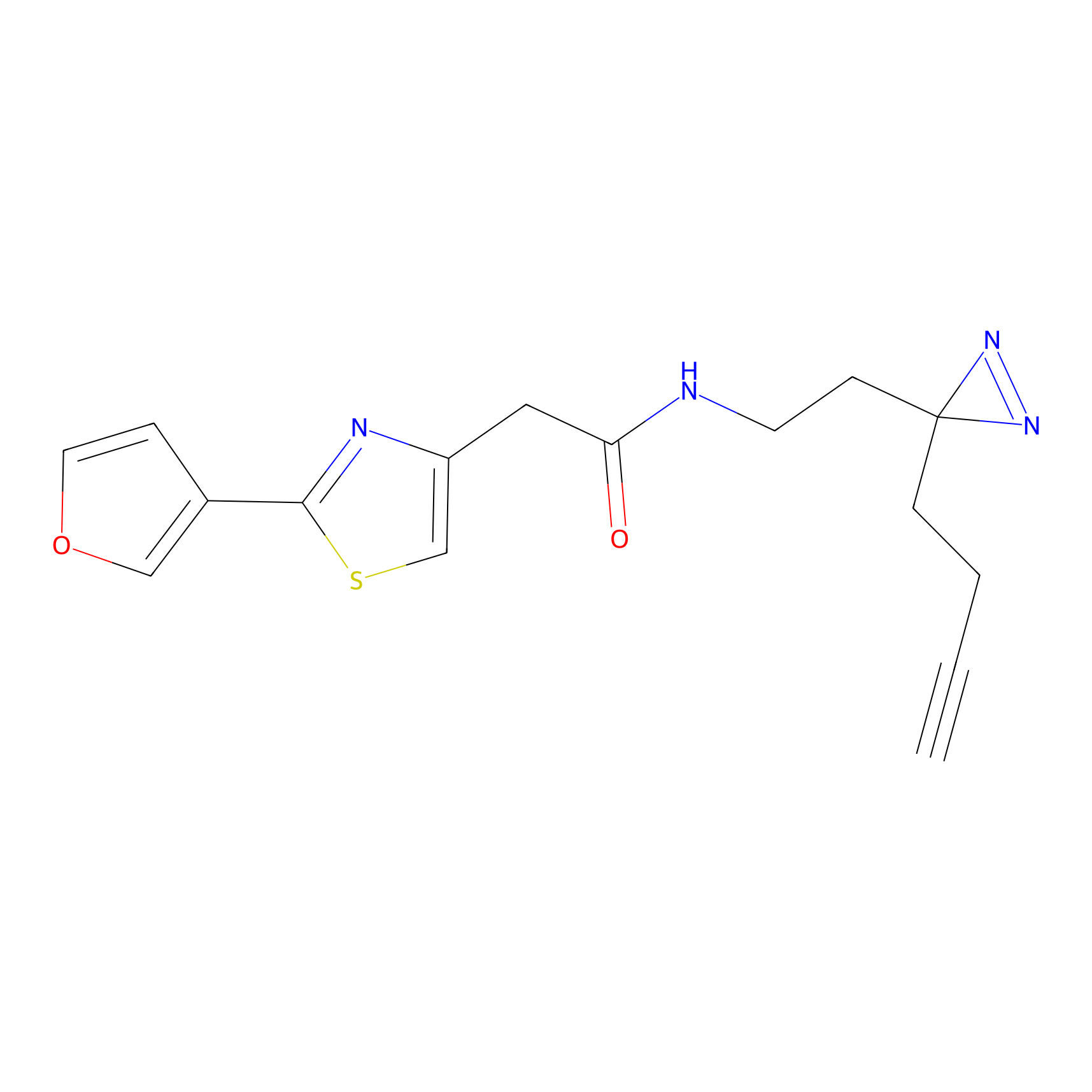
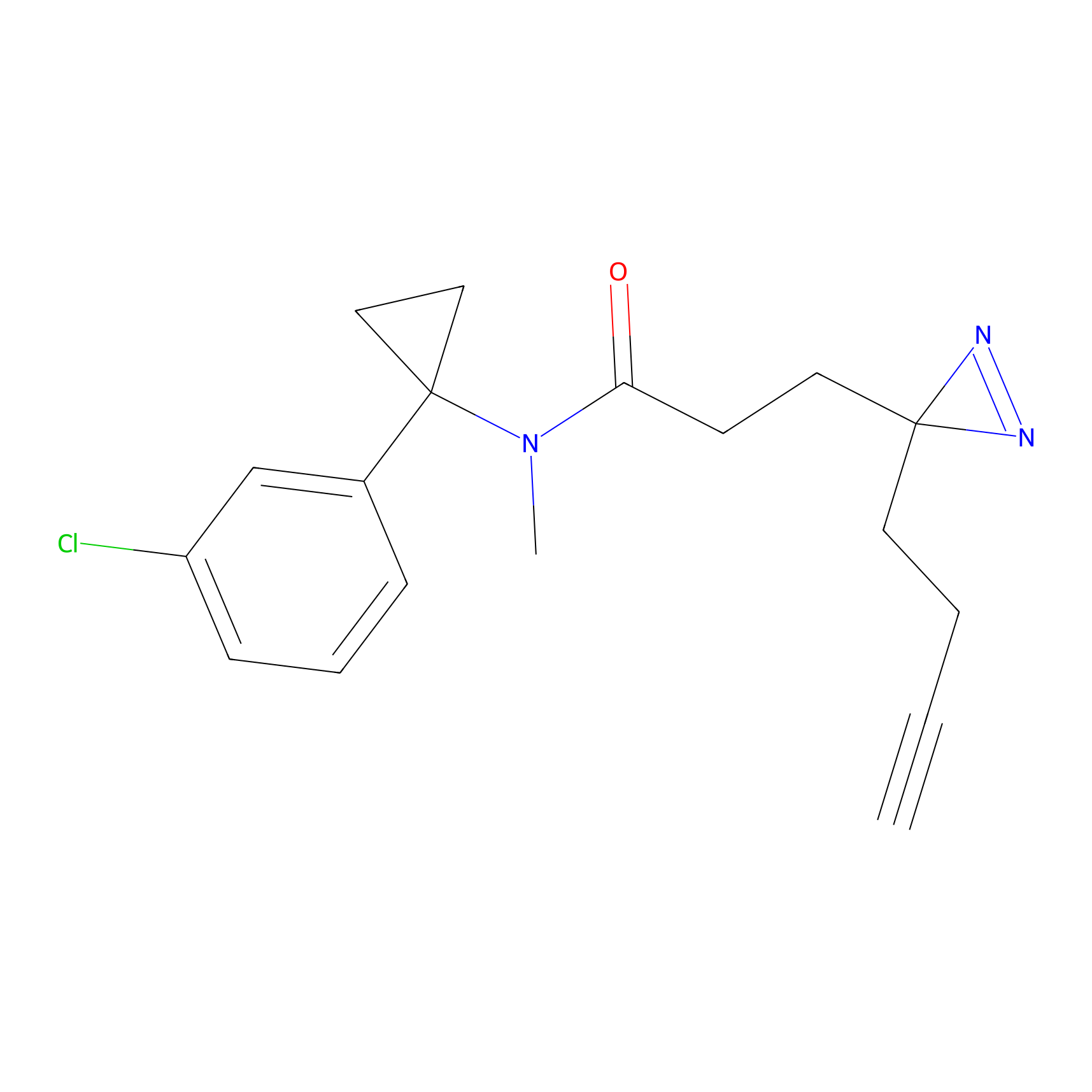
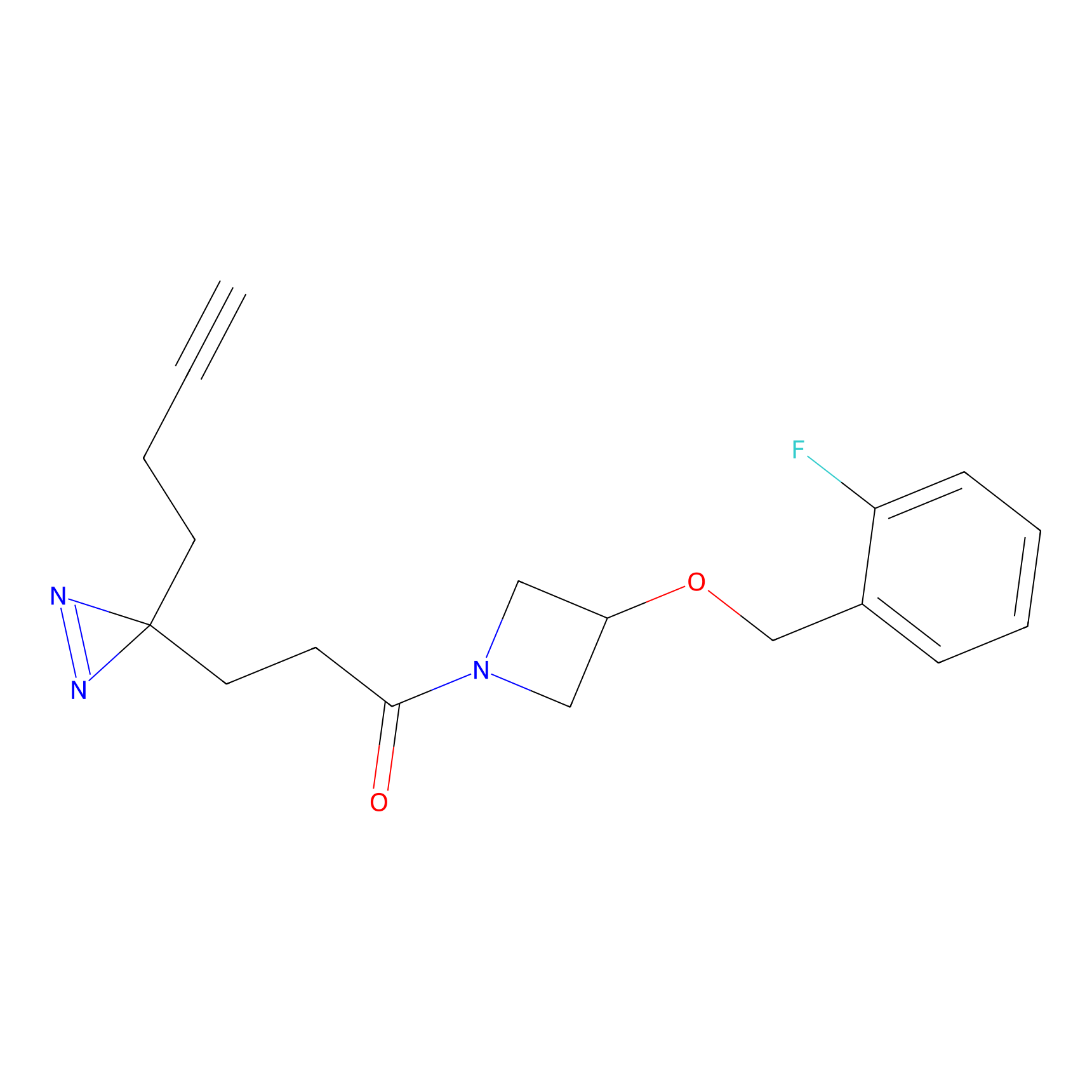
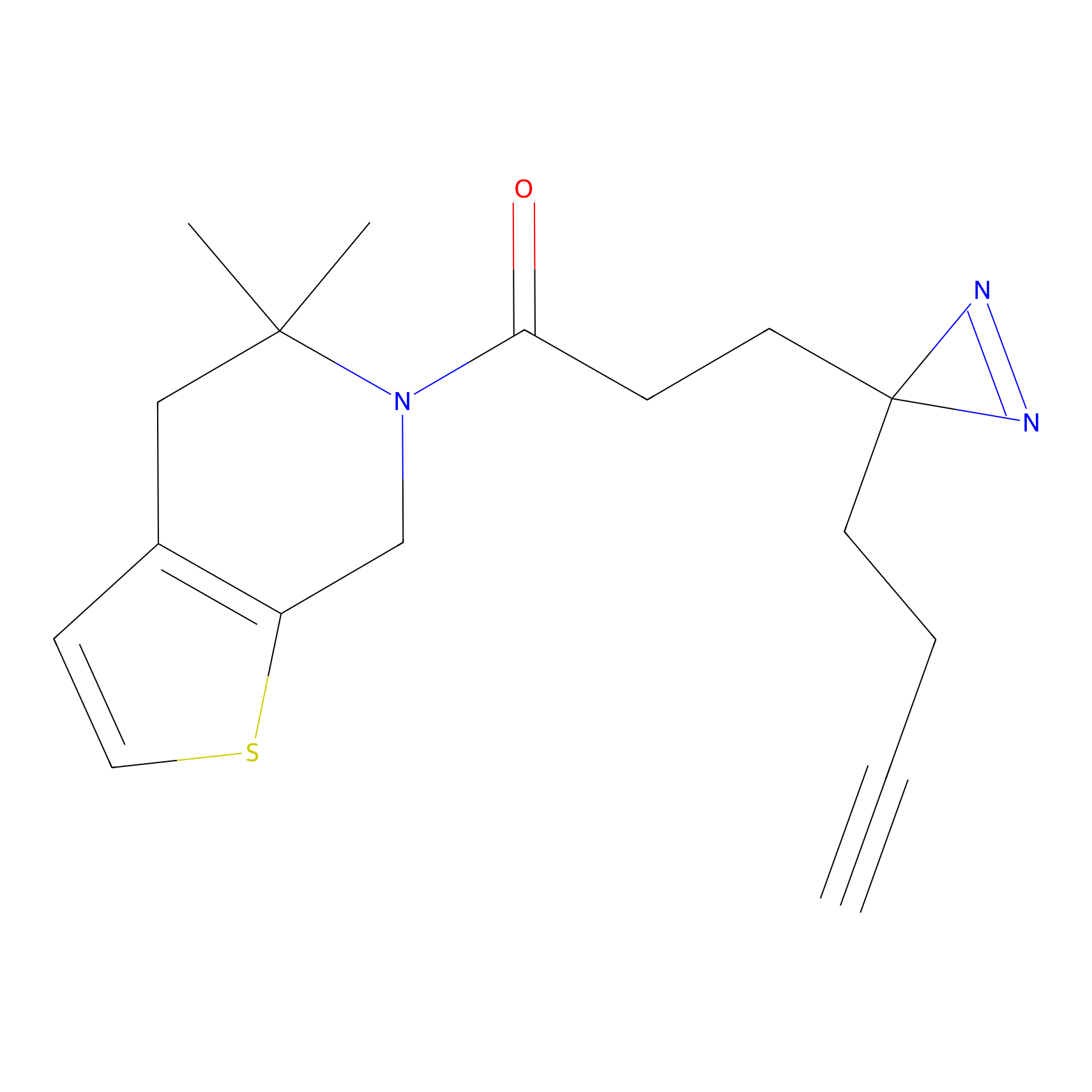
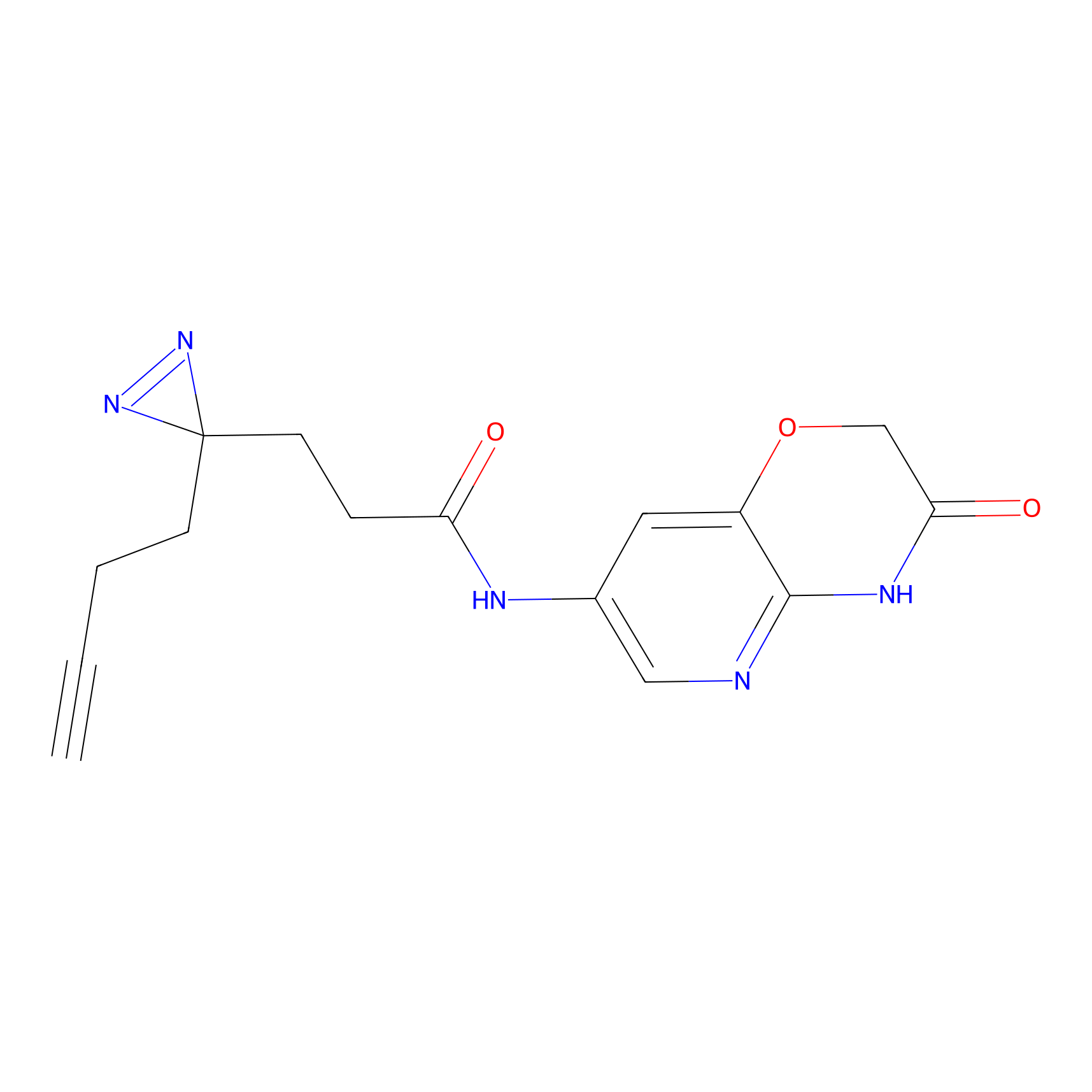
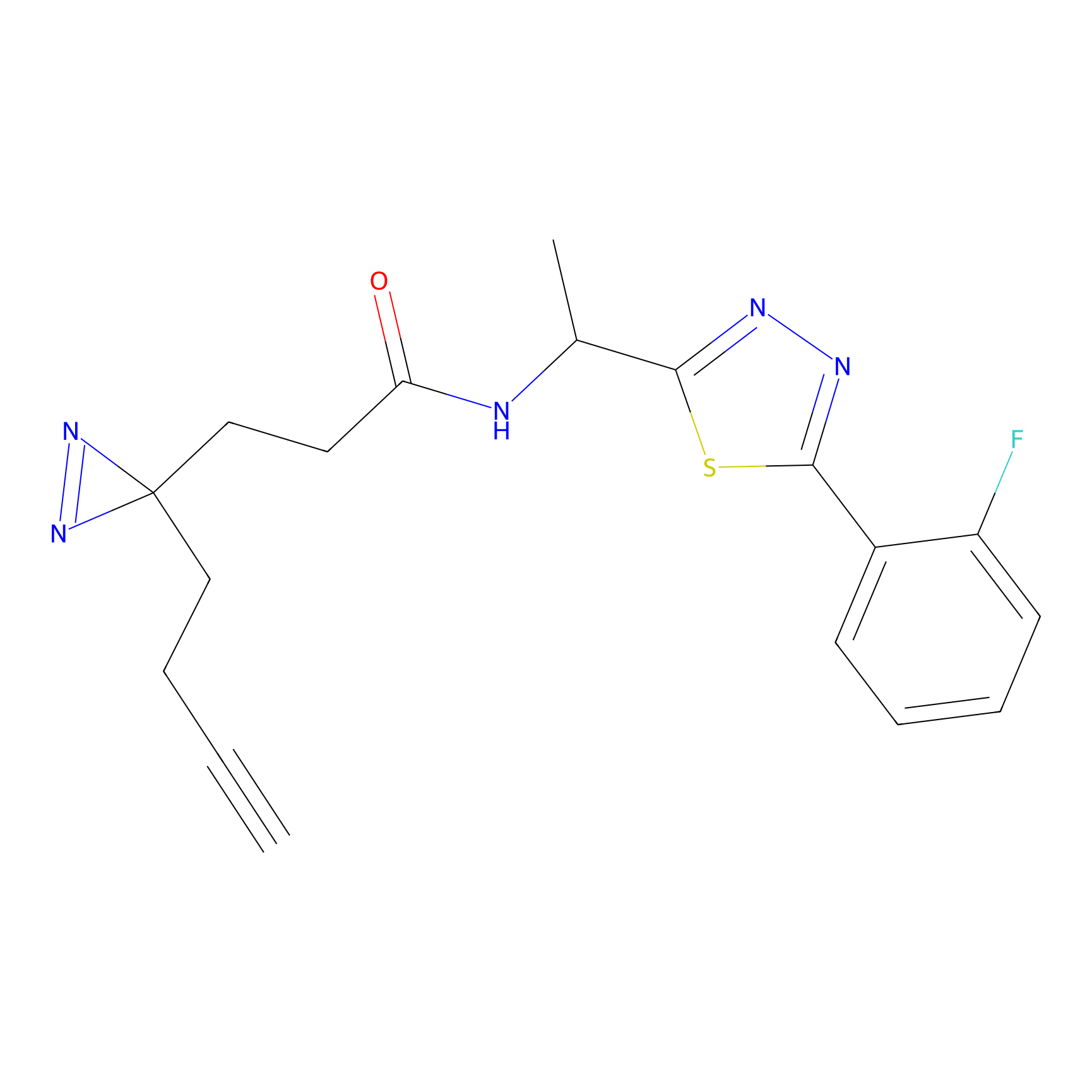
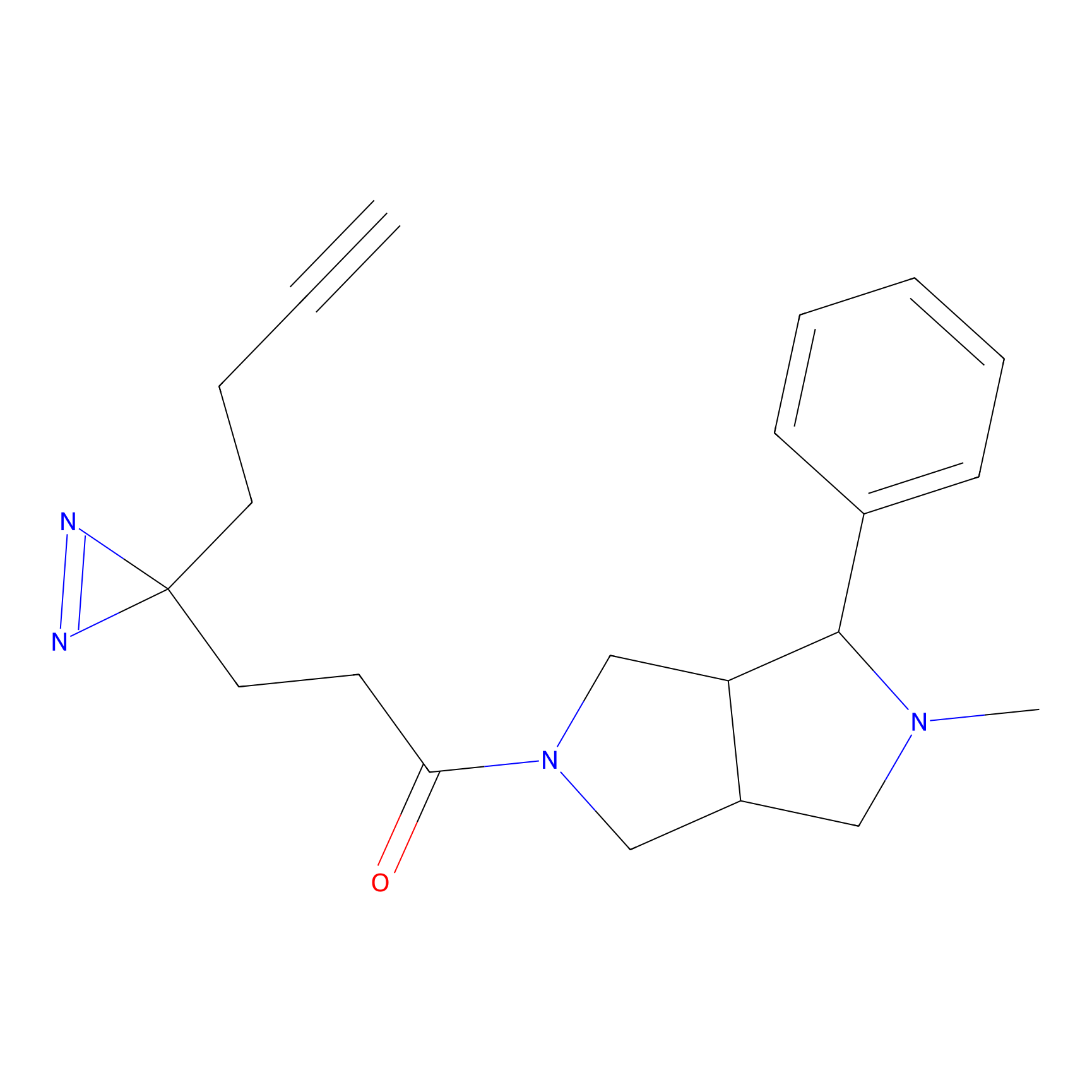
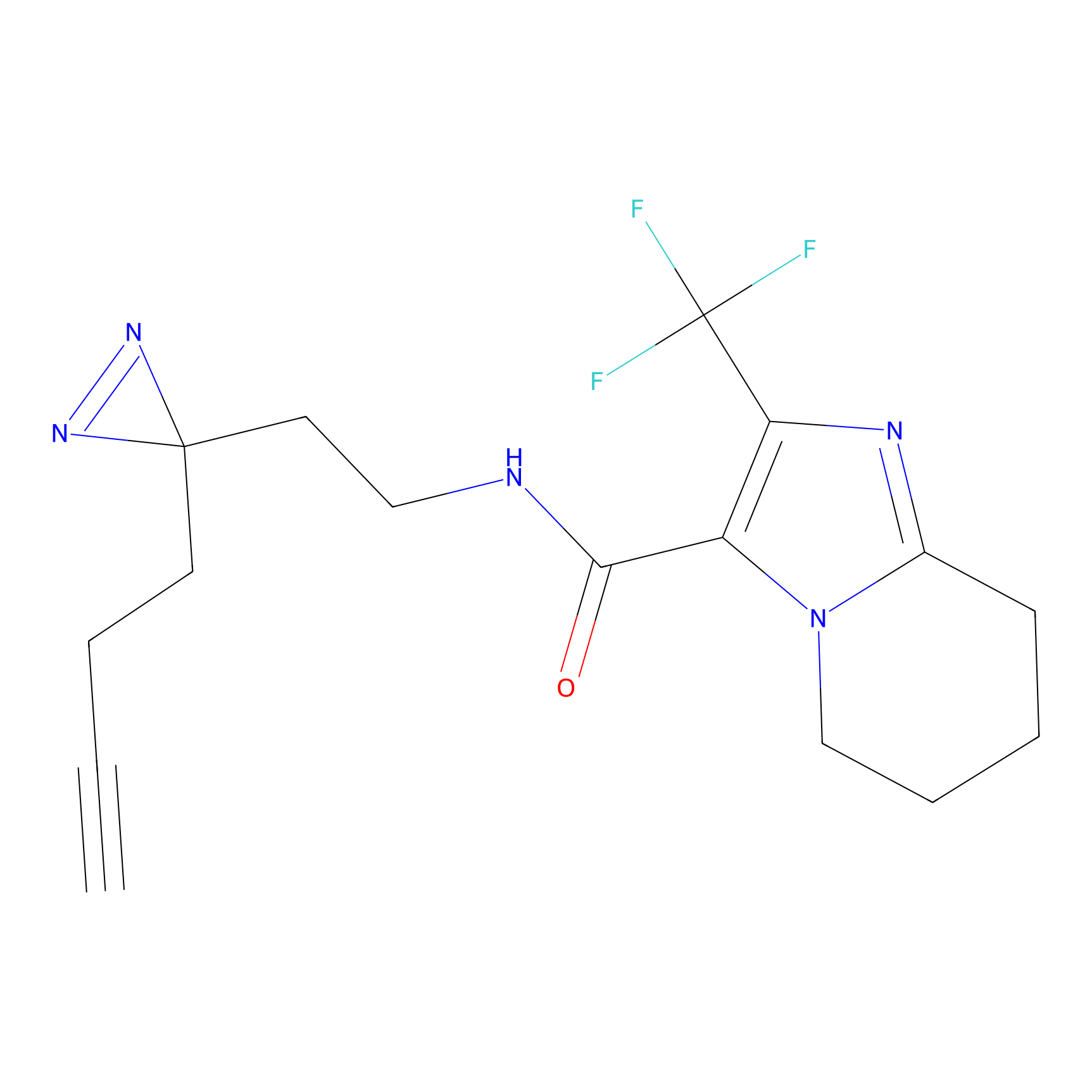
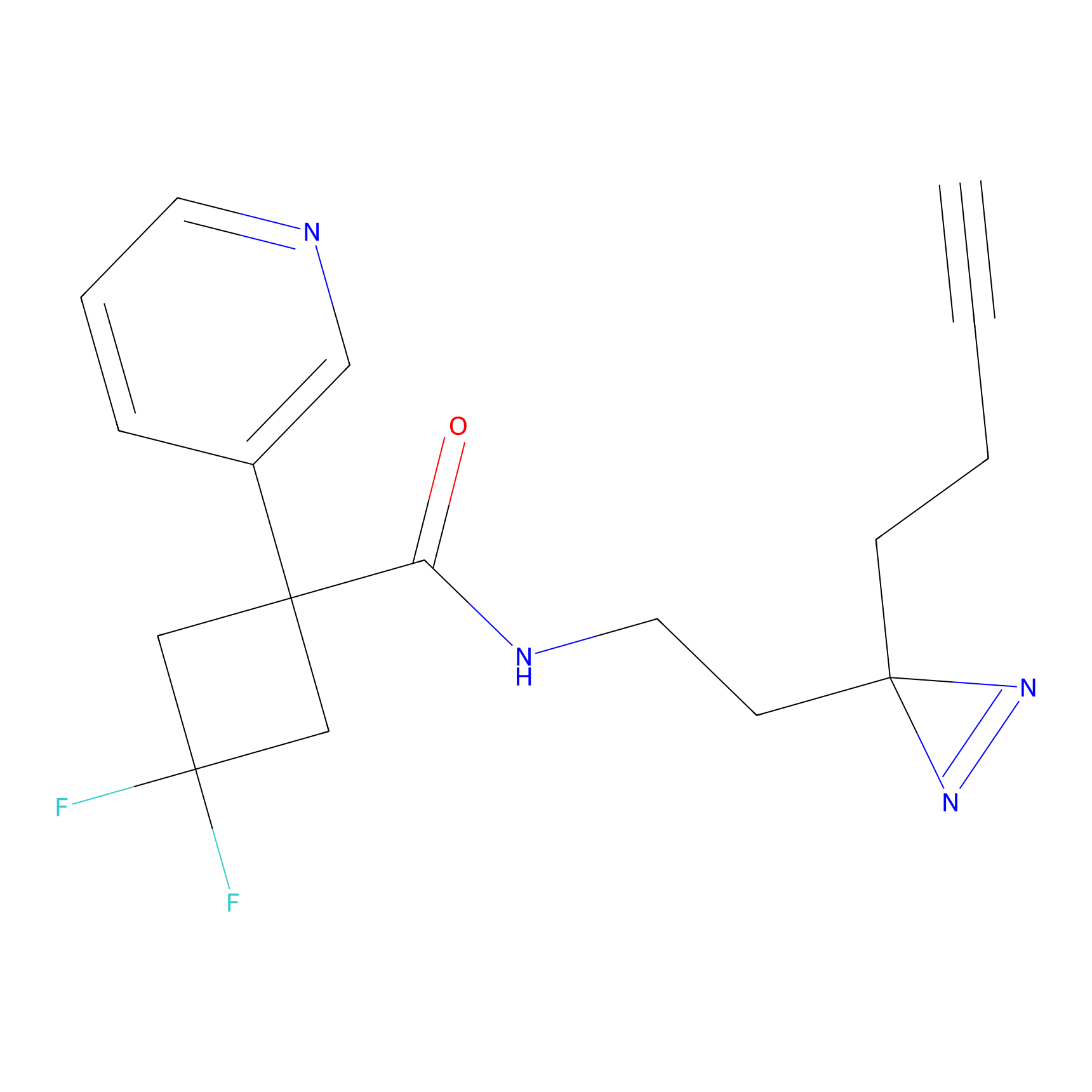
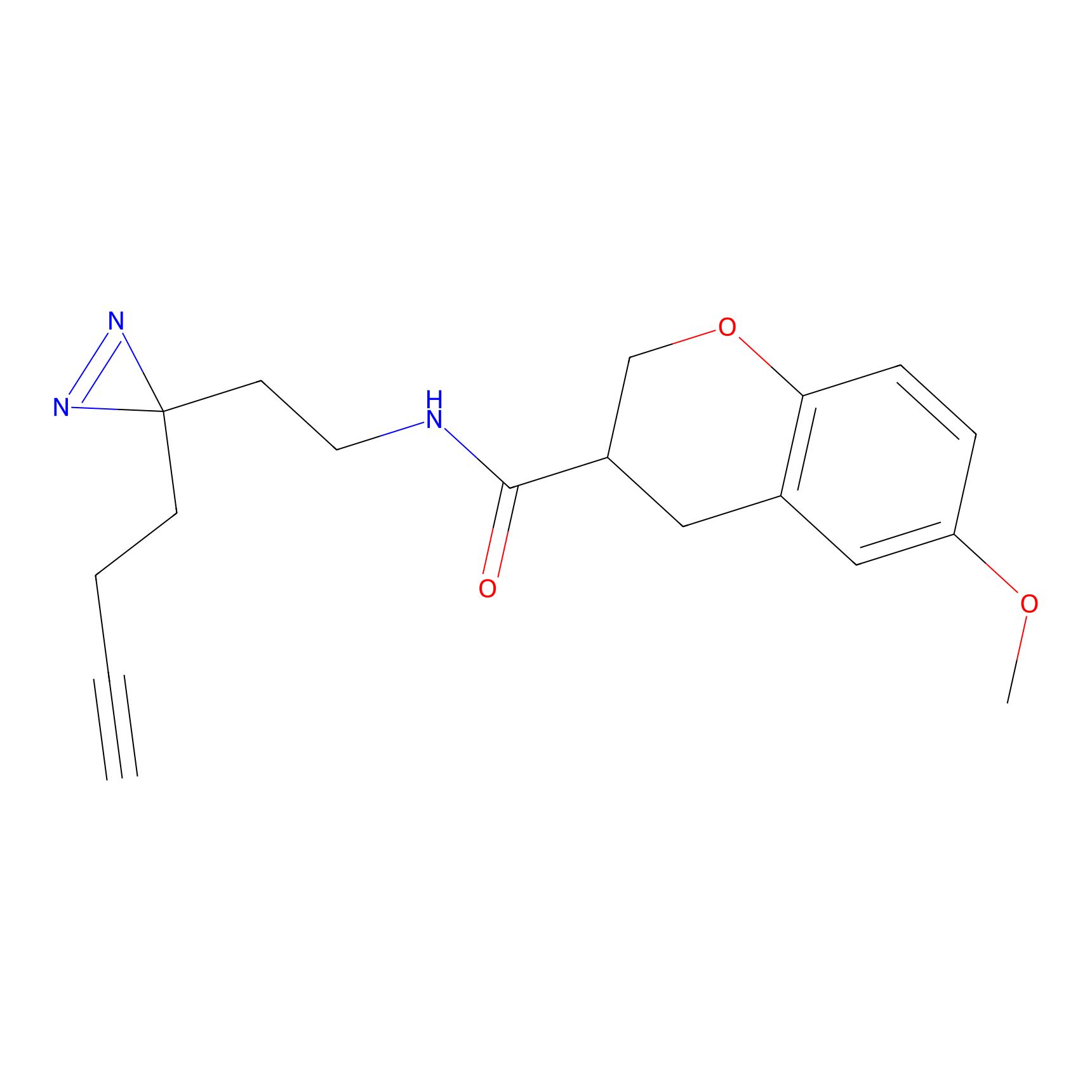
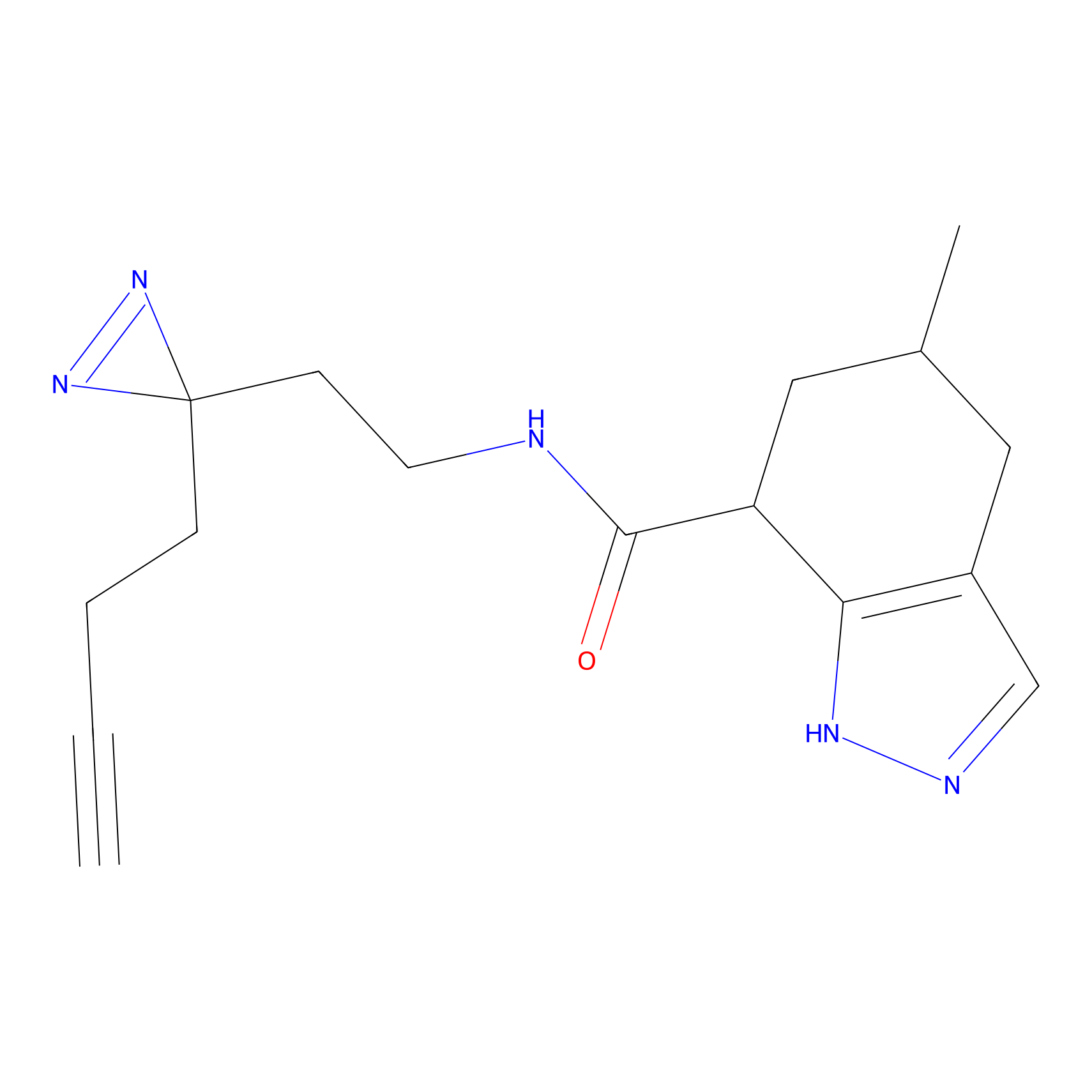
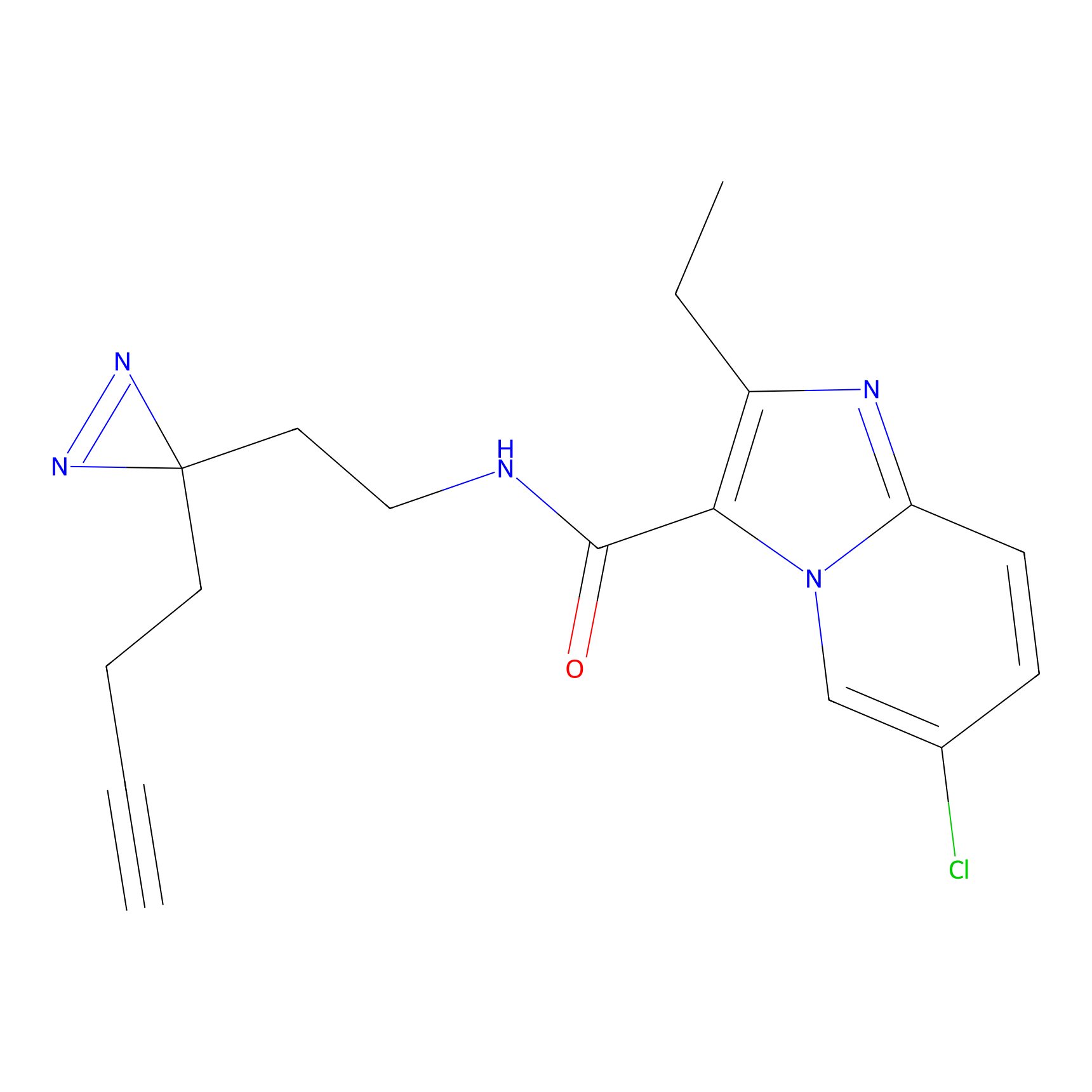
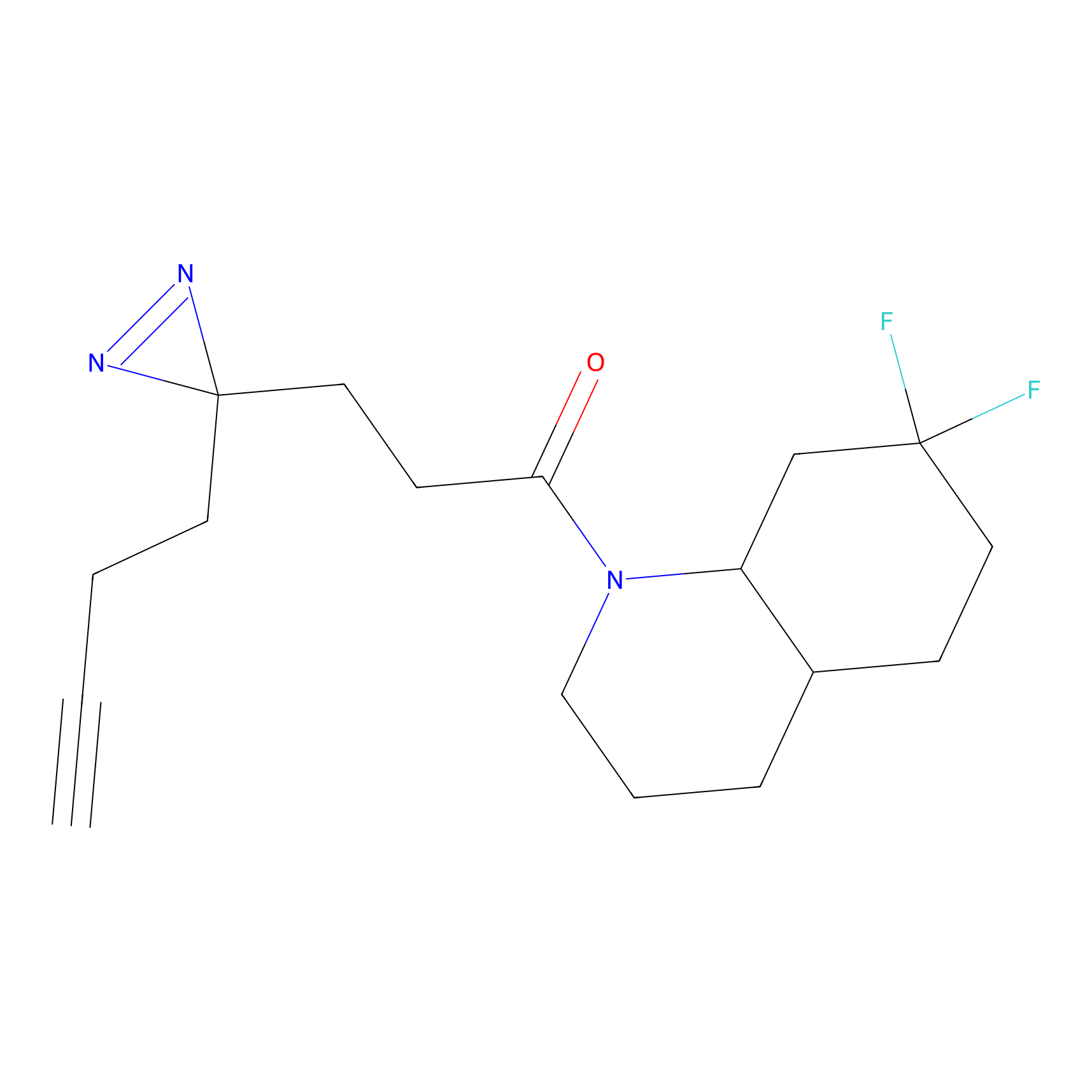
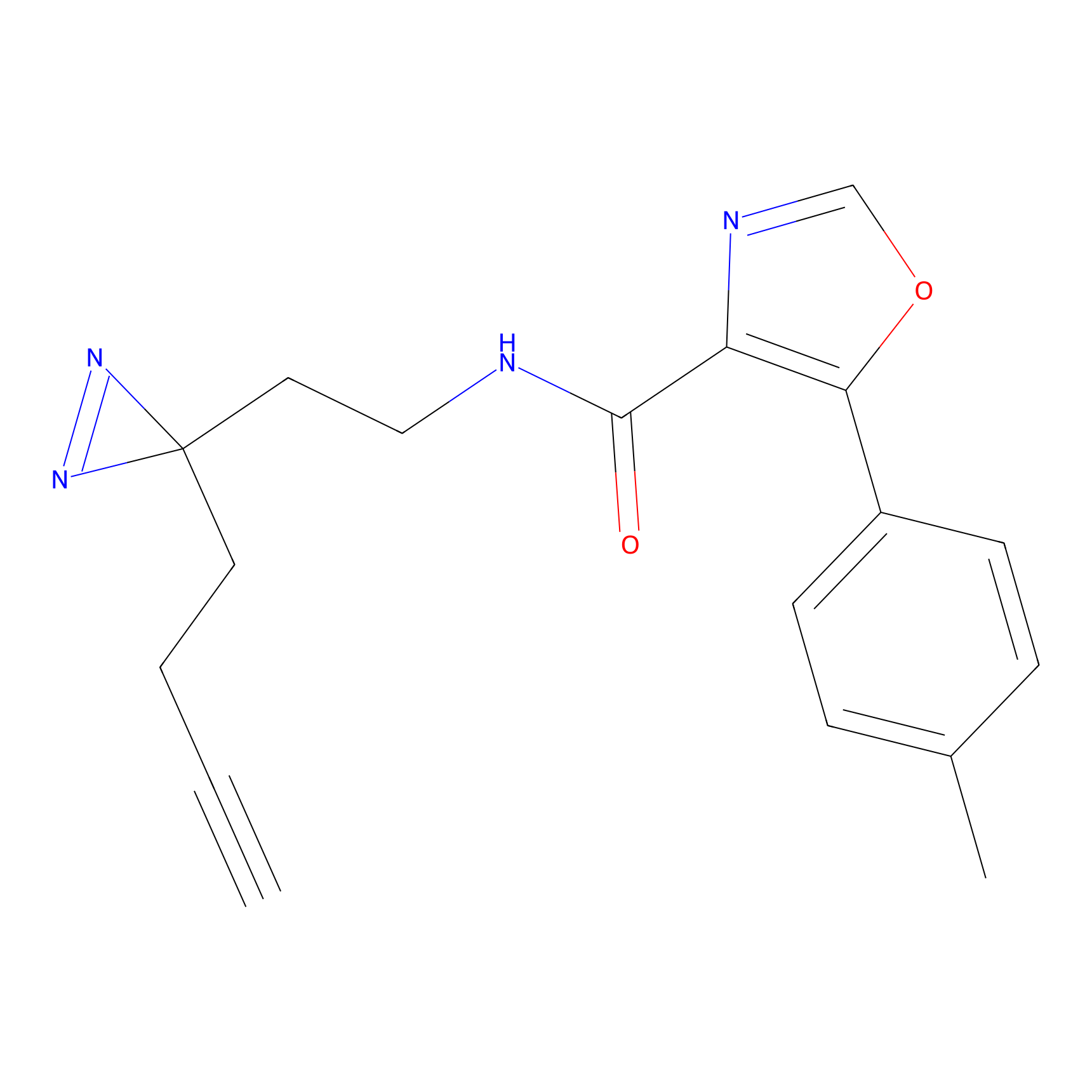
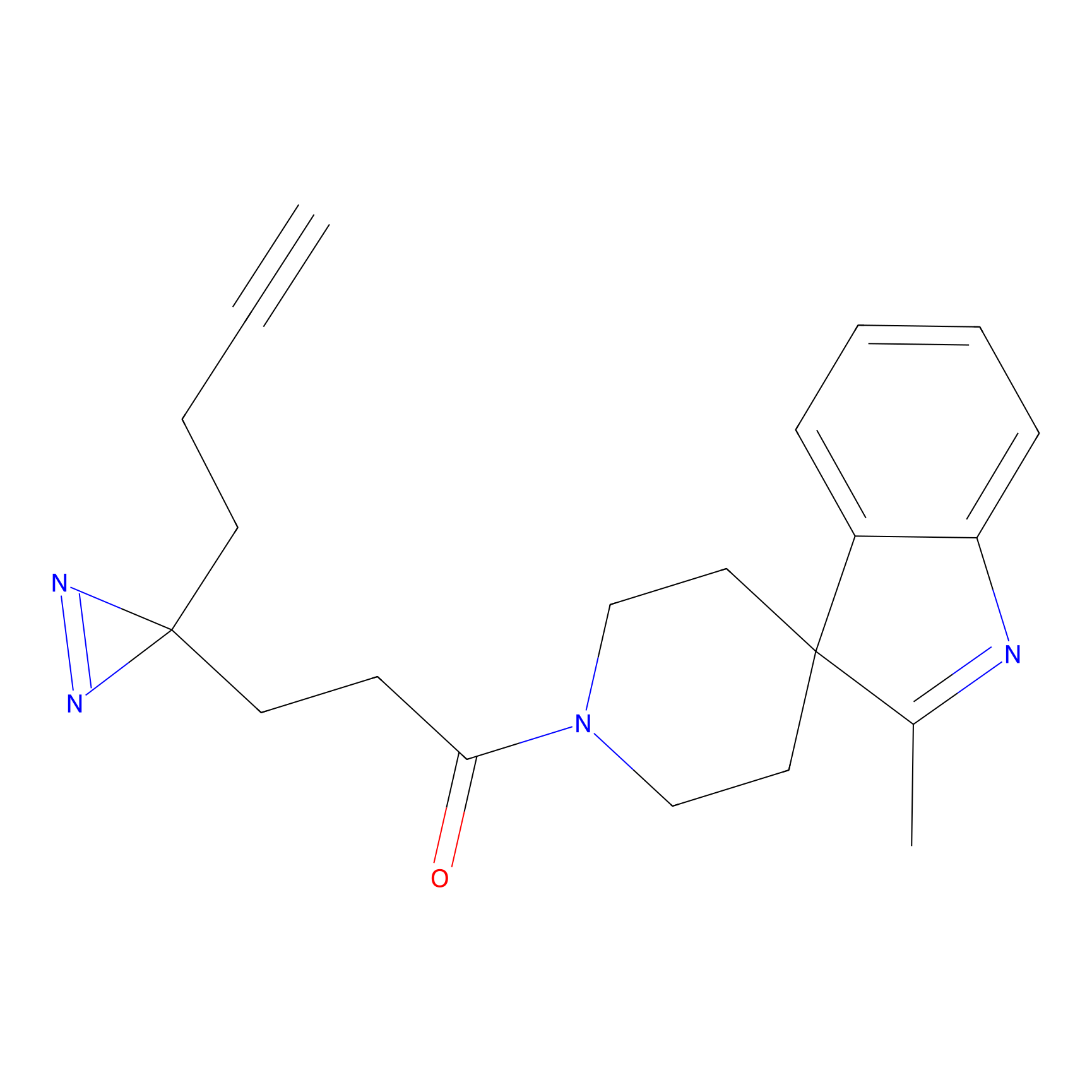
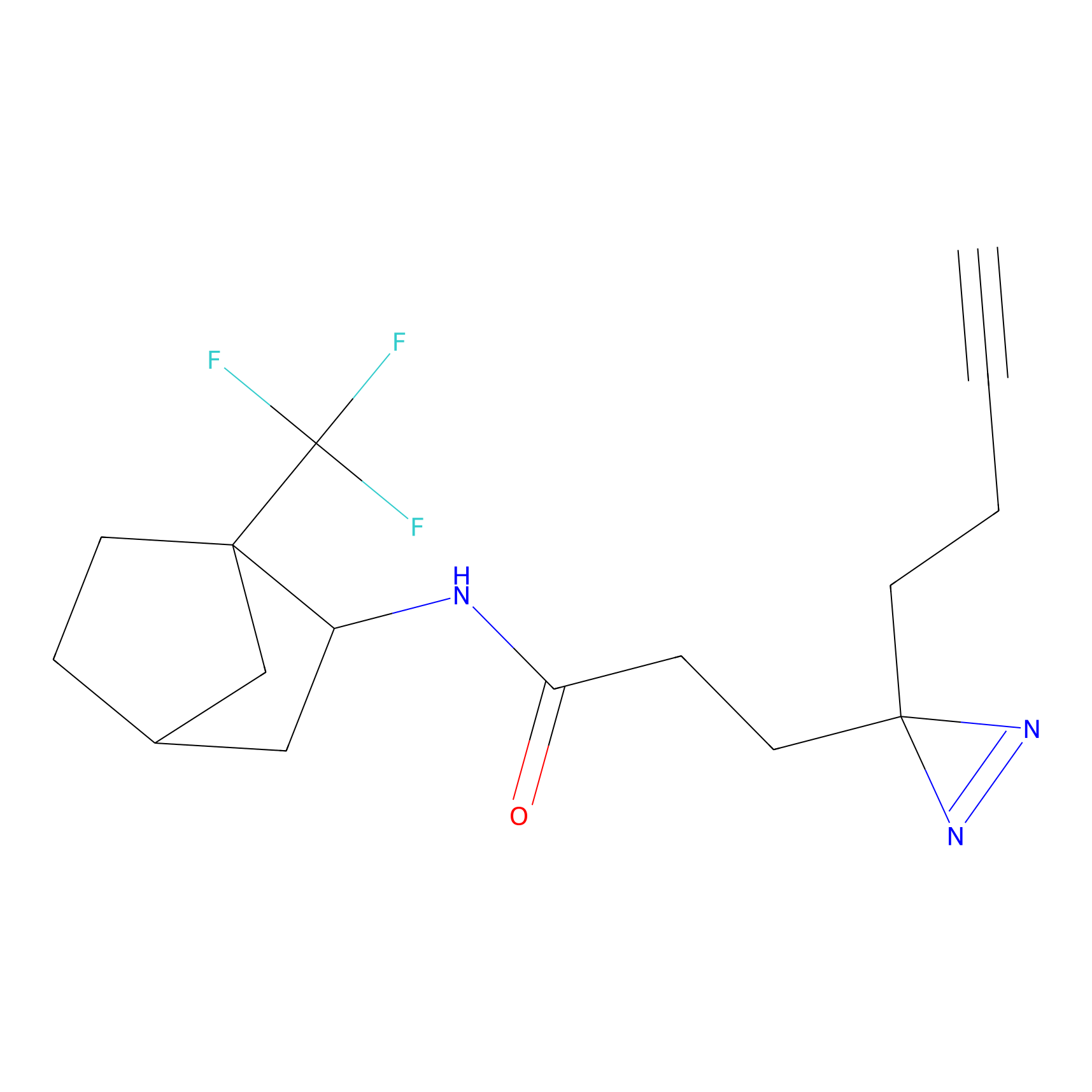
|
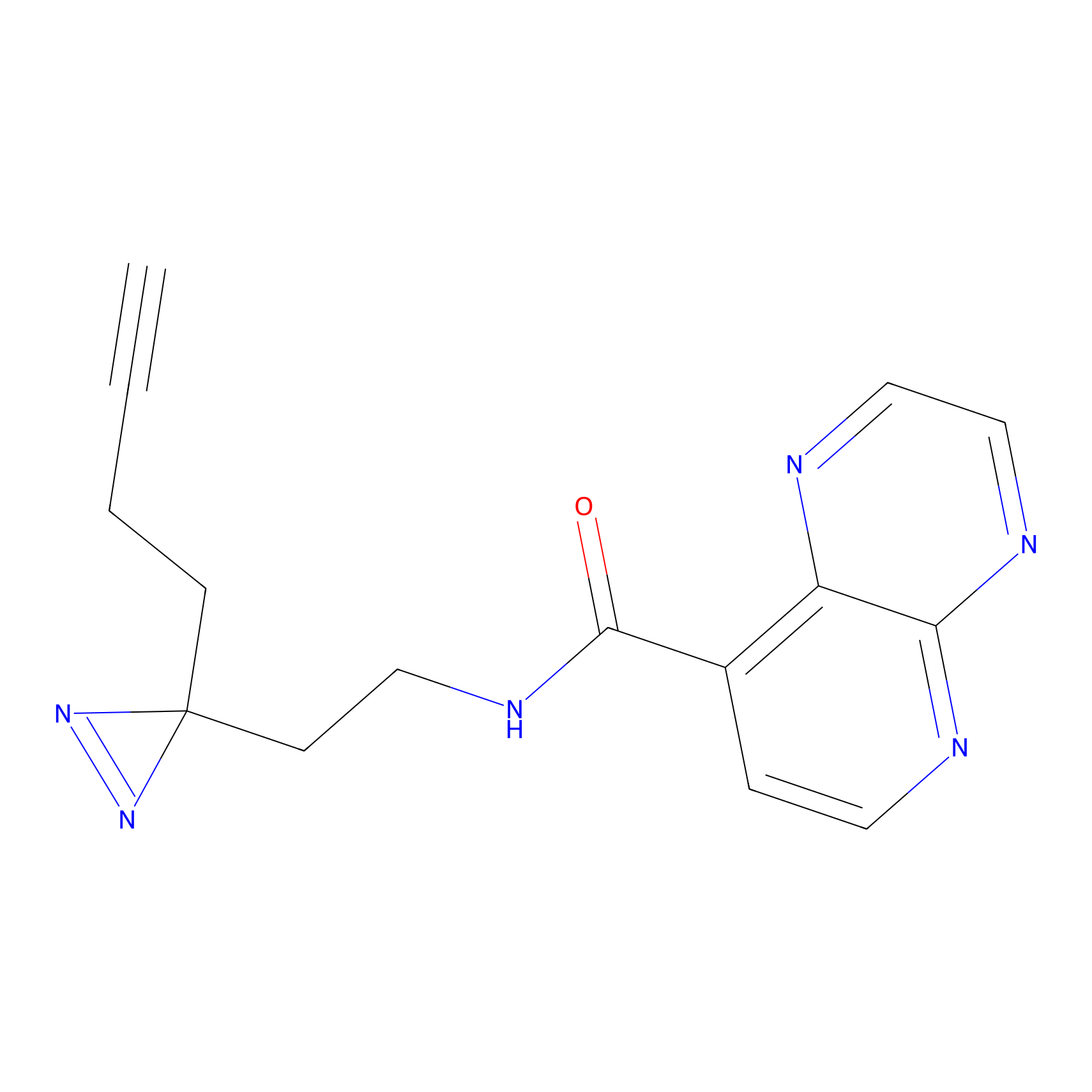
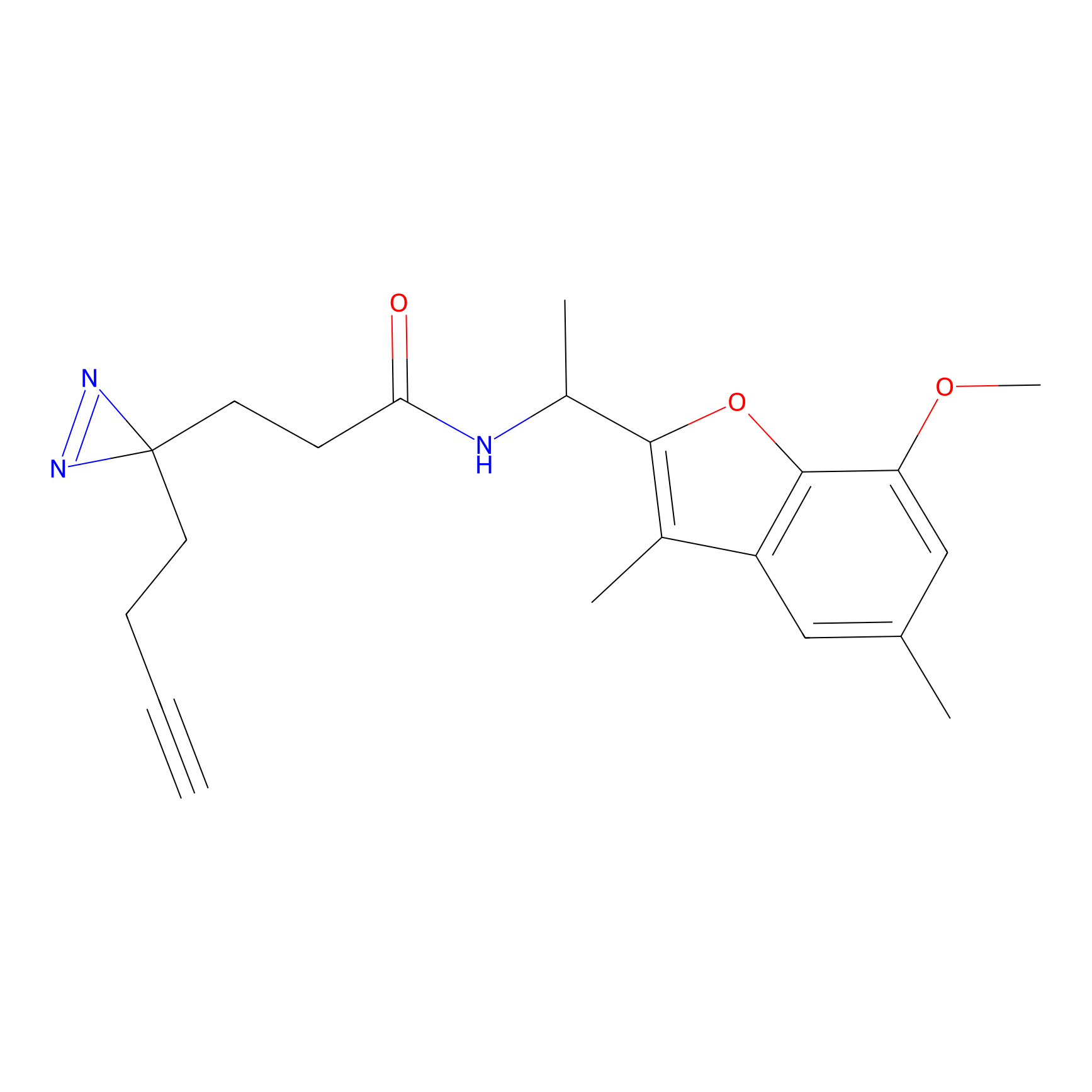
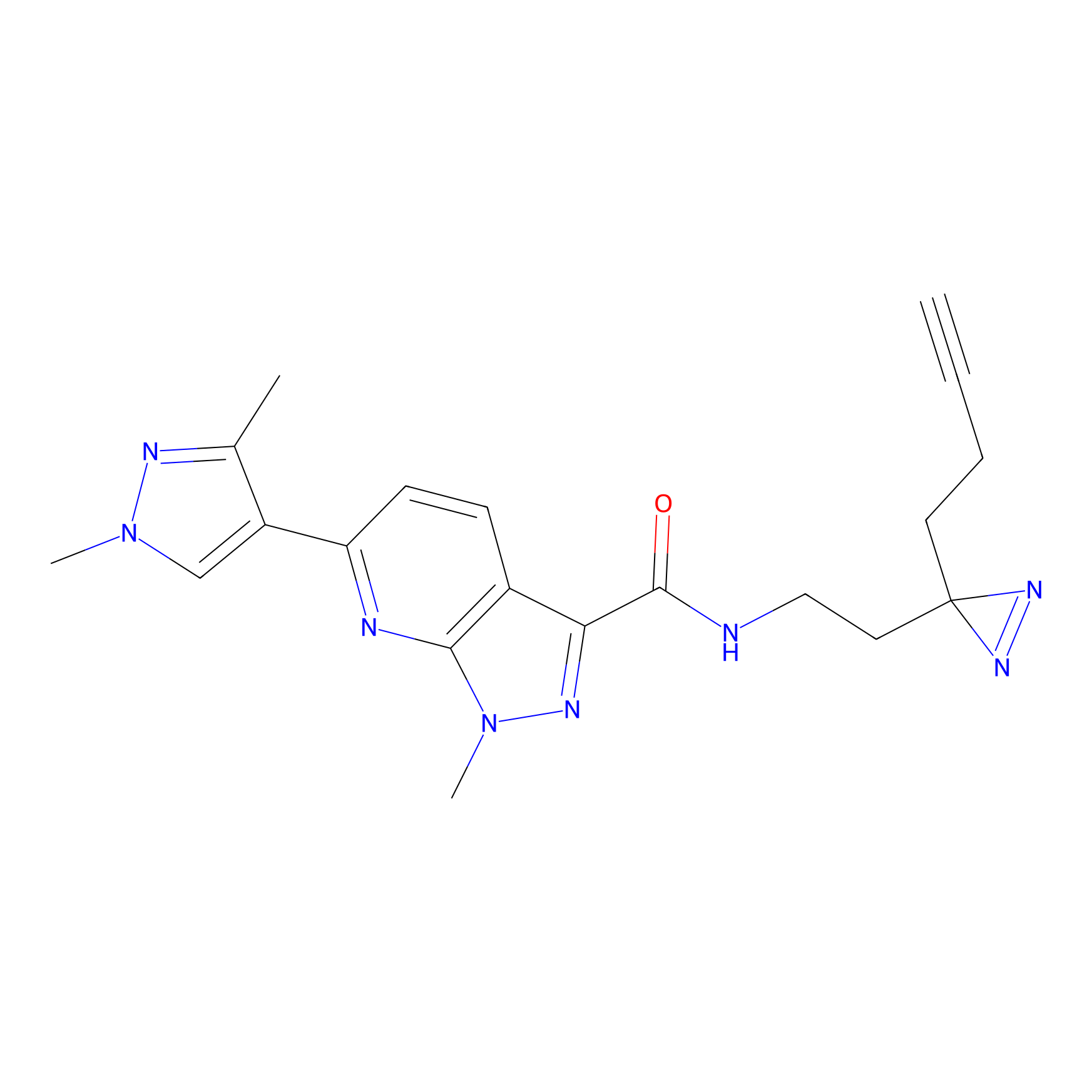
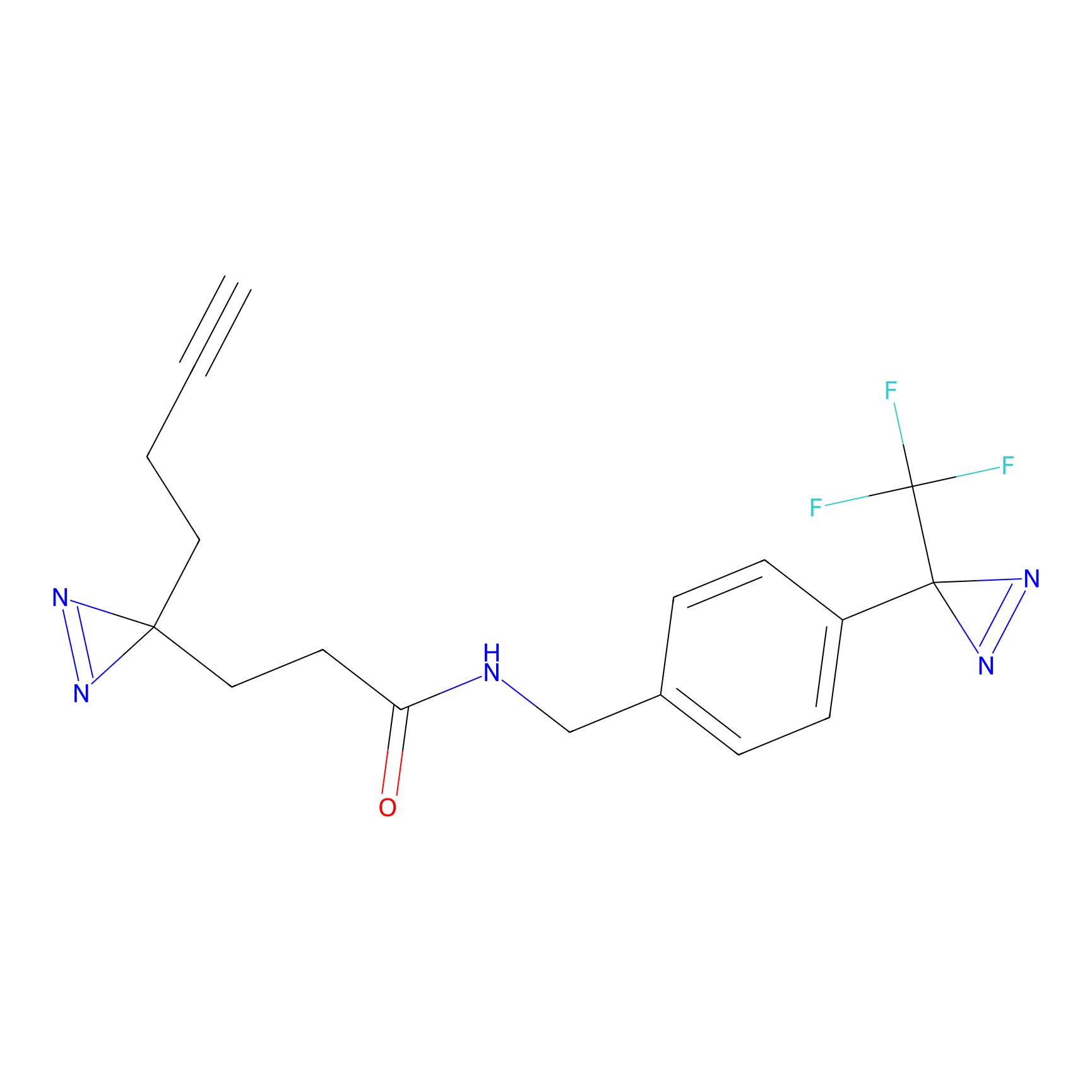
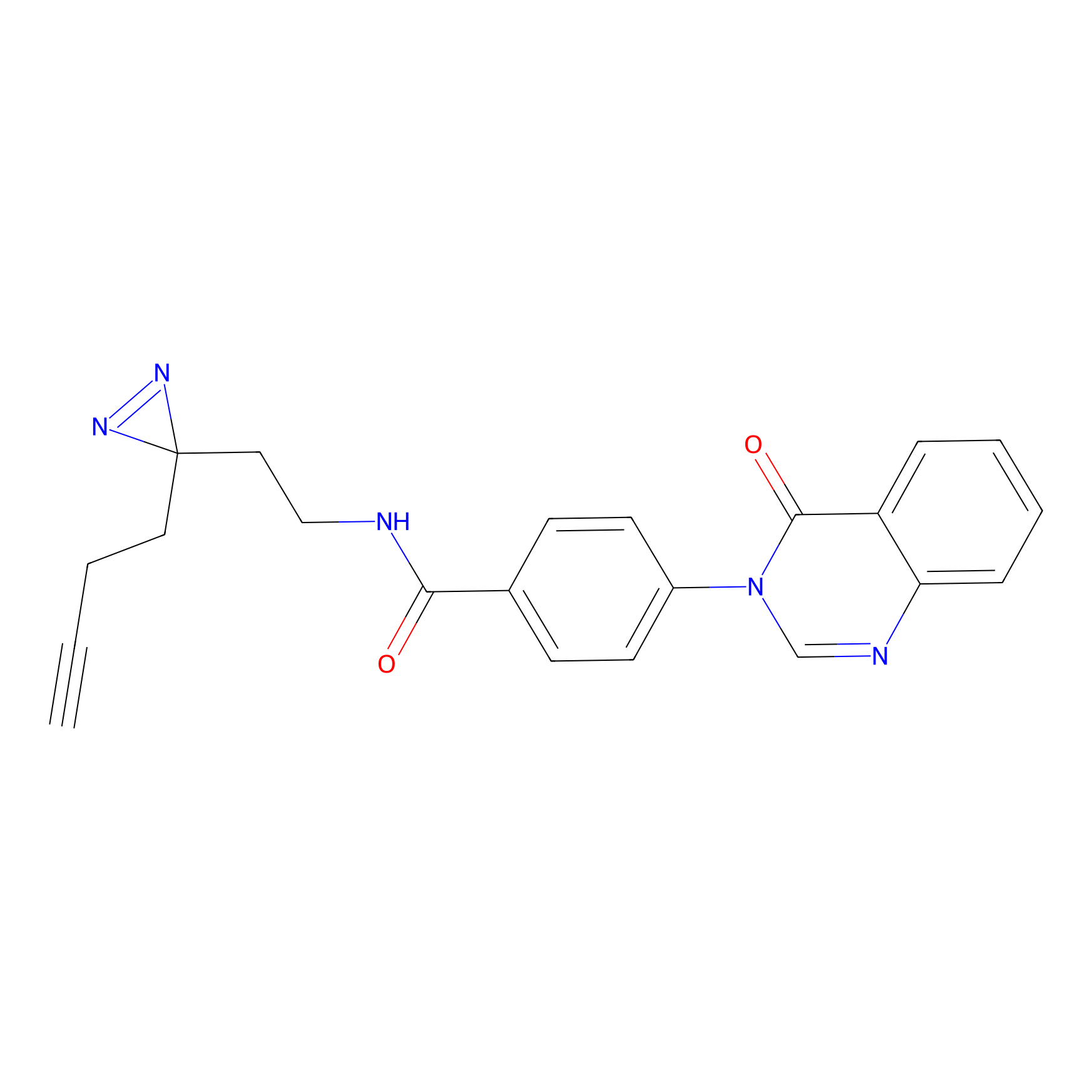
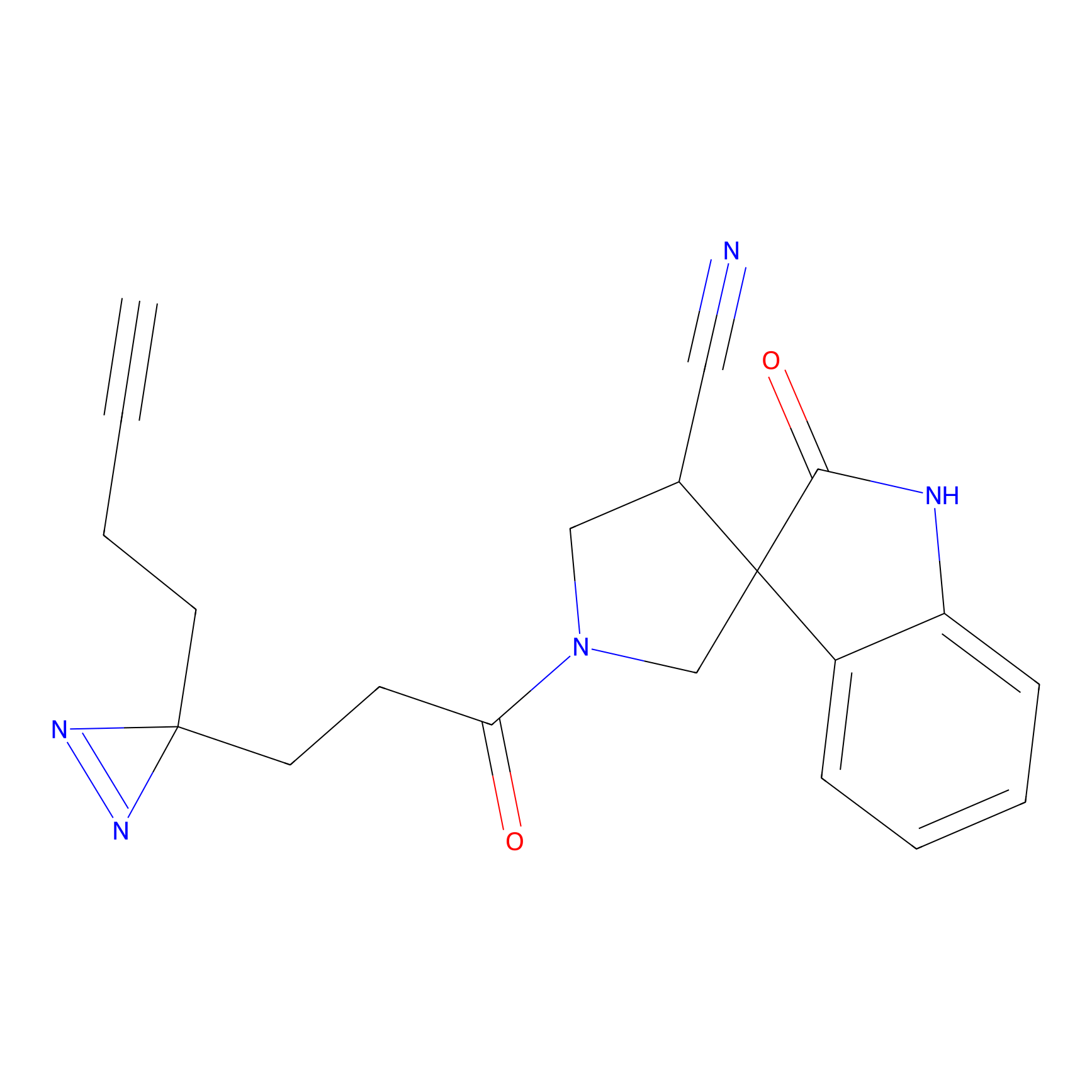
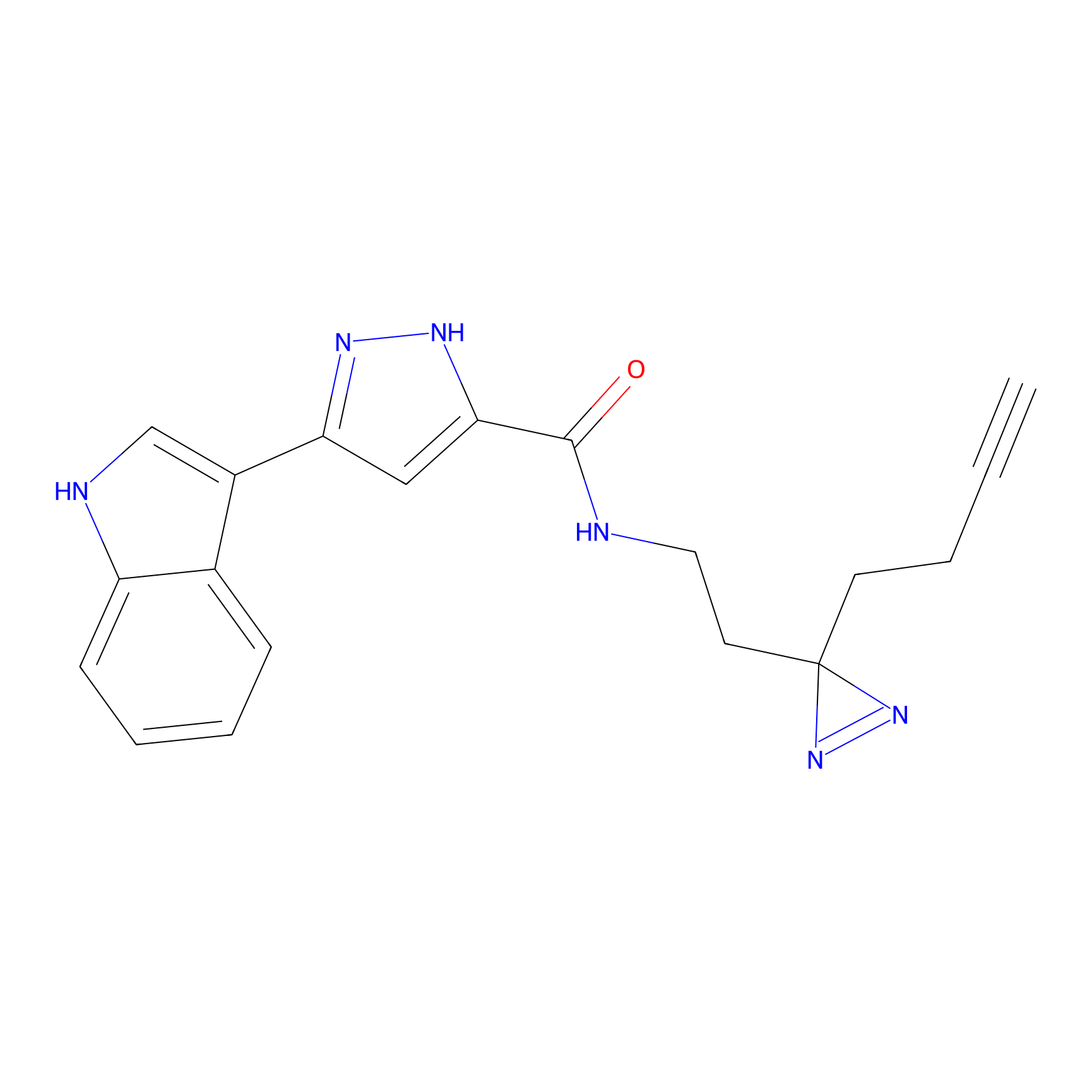
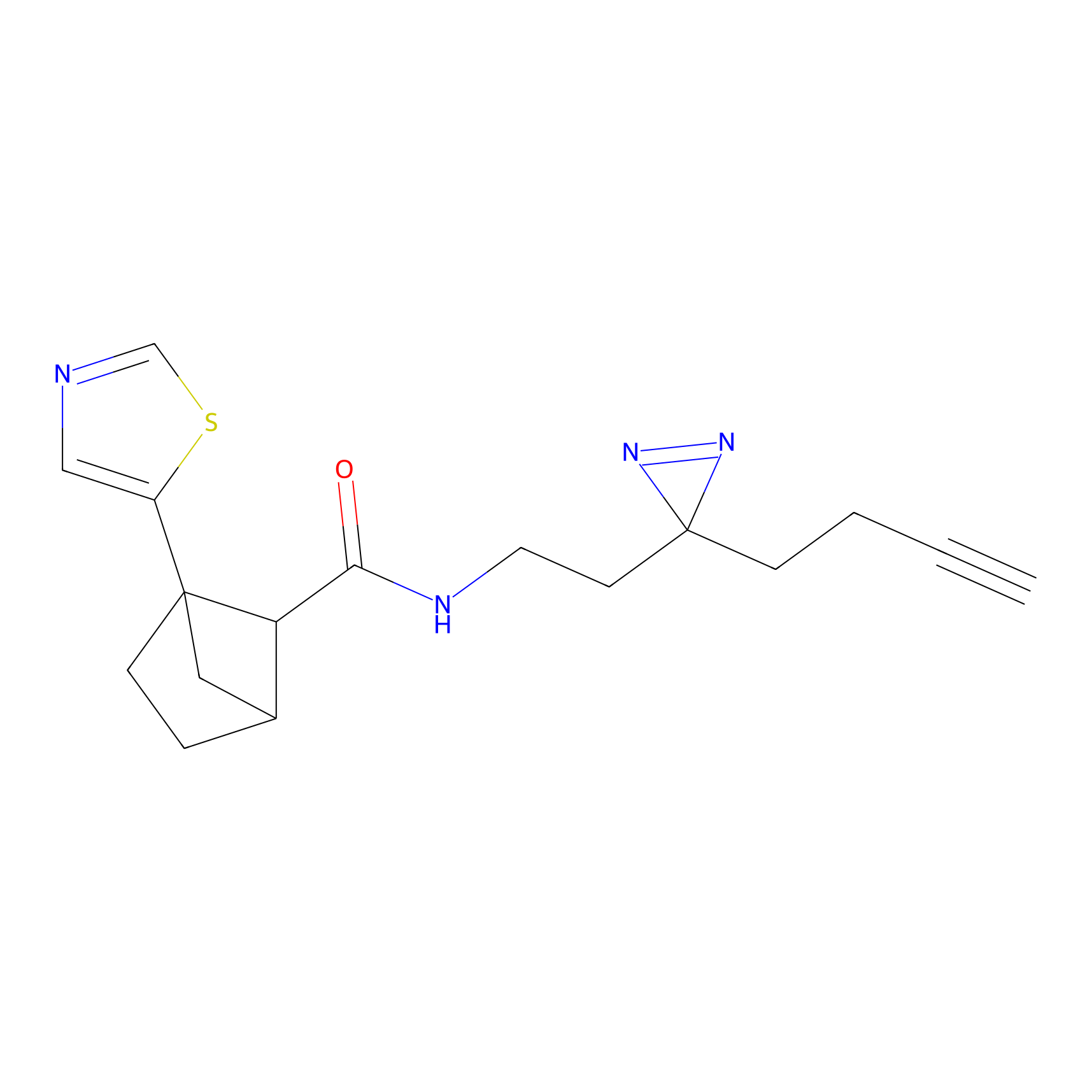
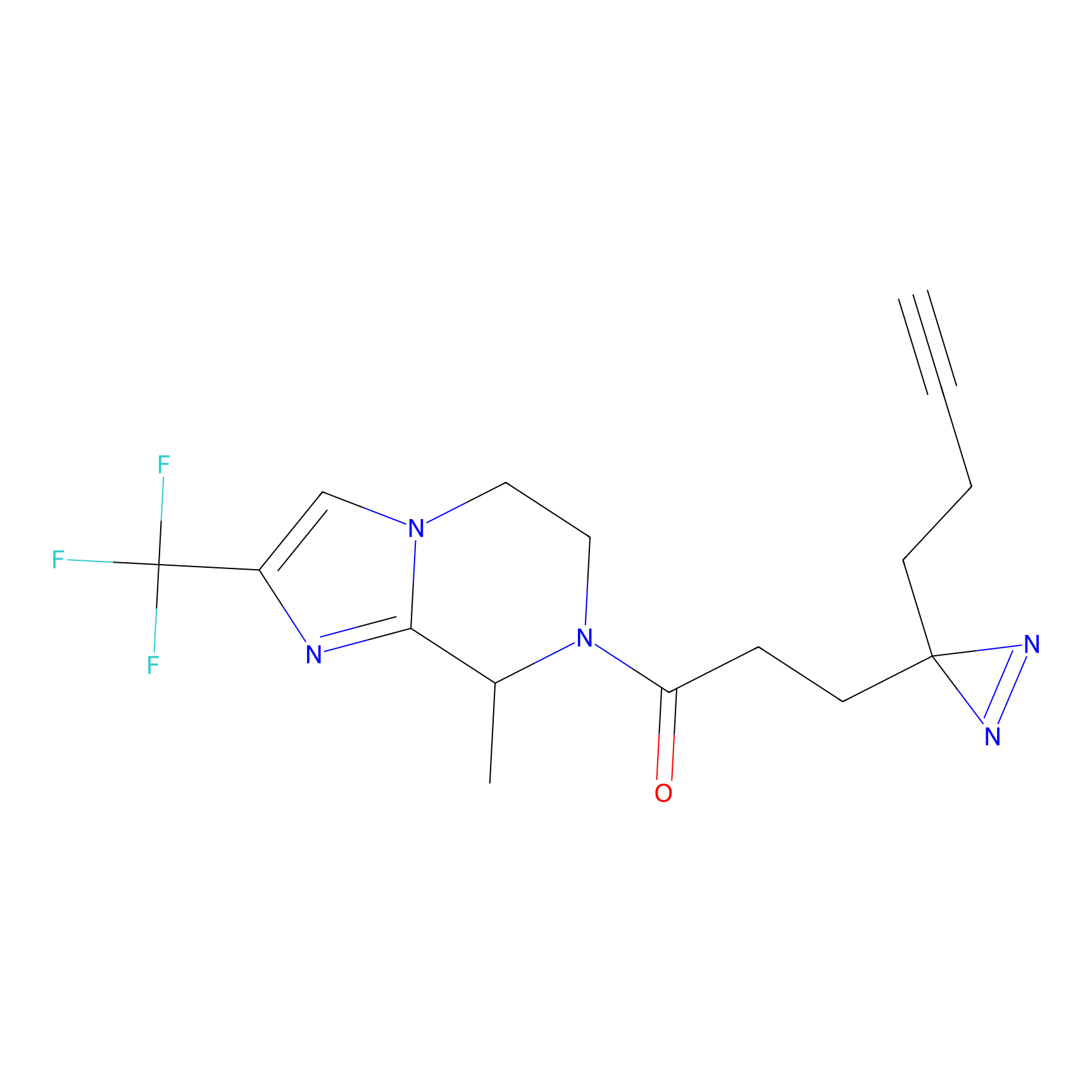
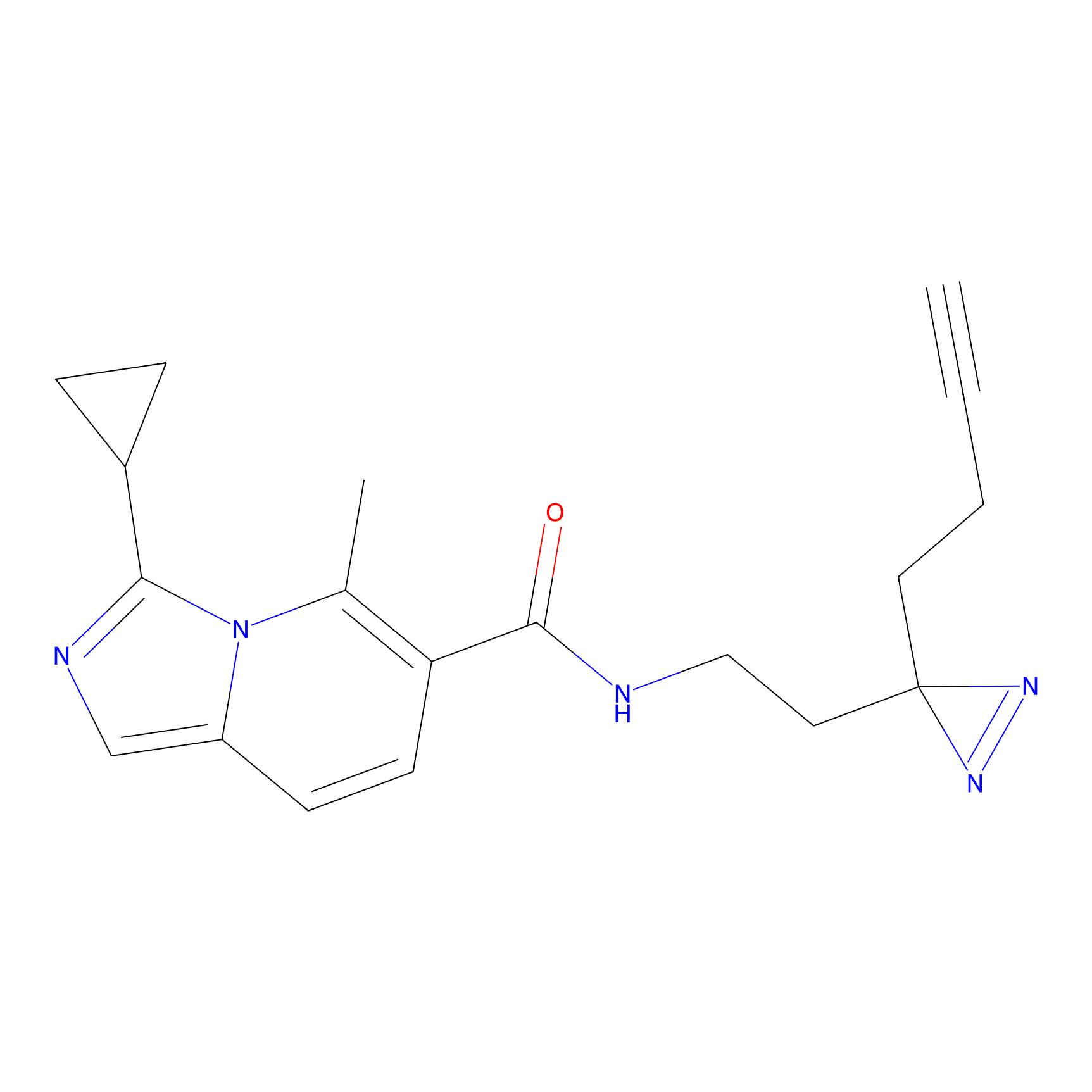
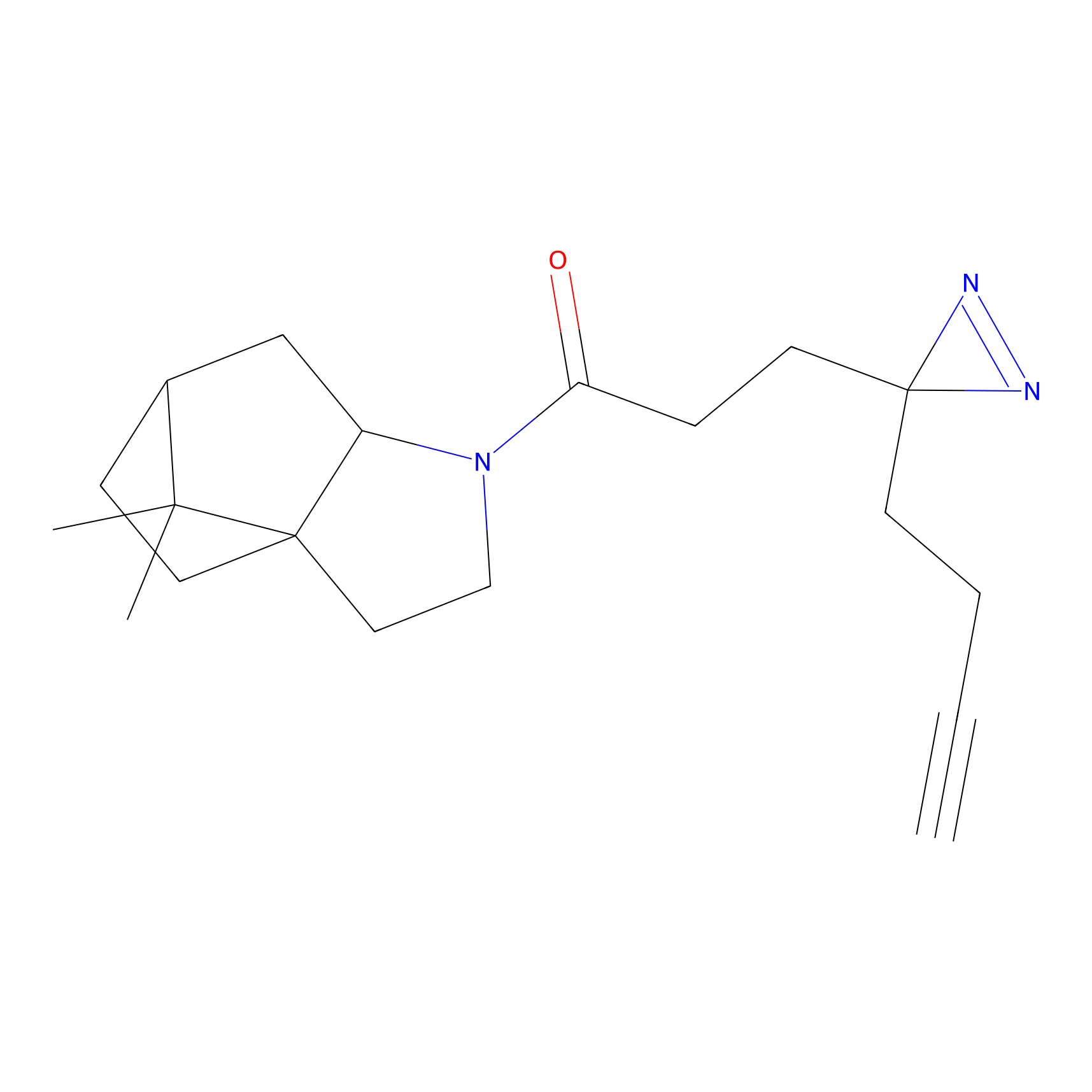
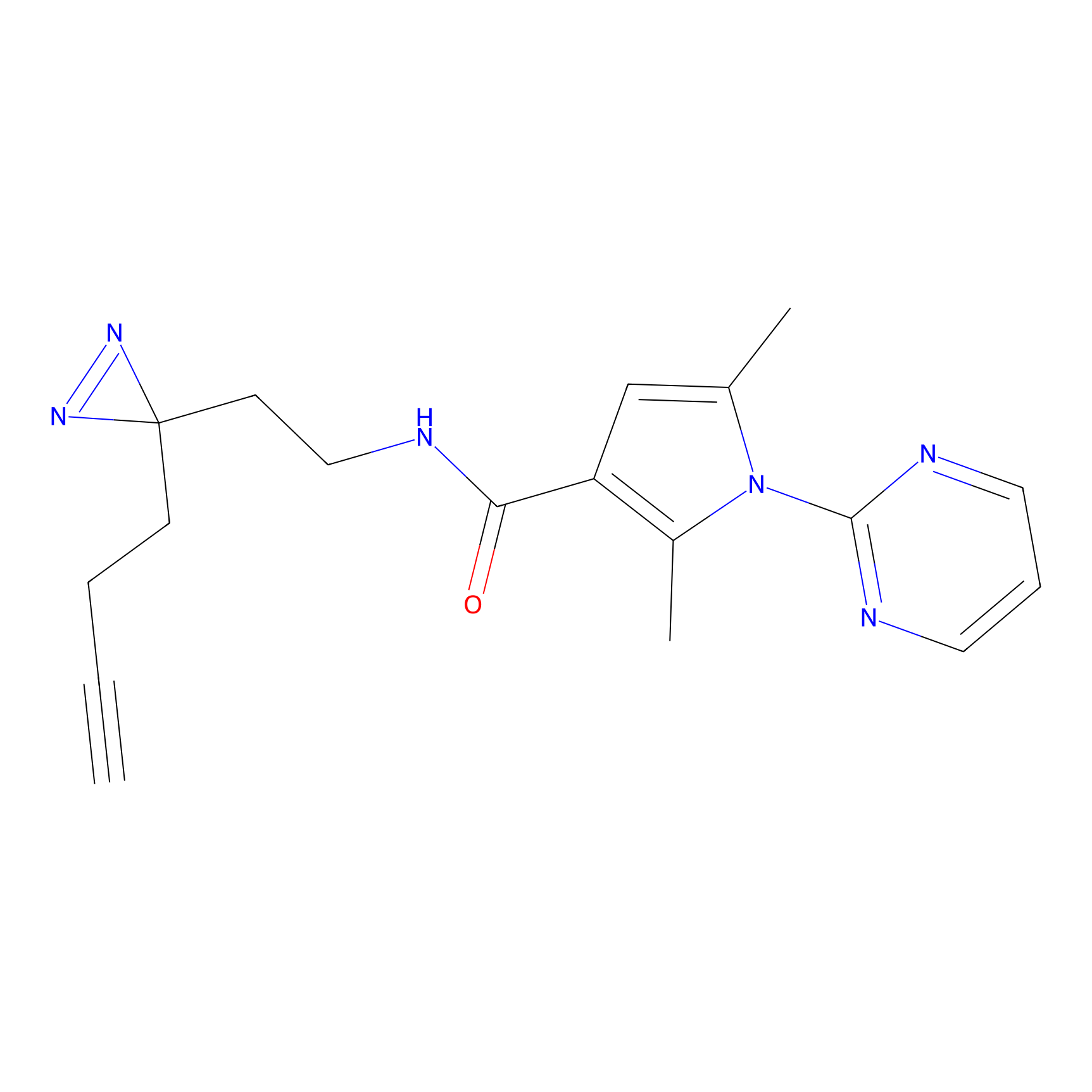
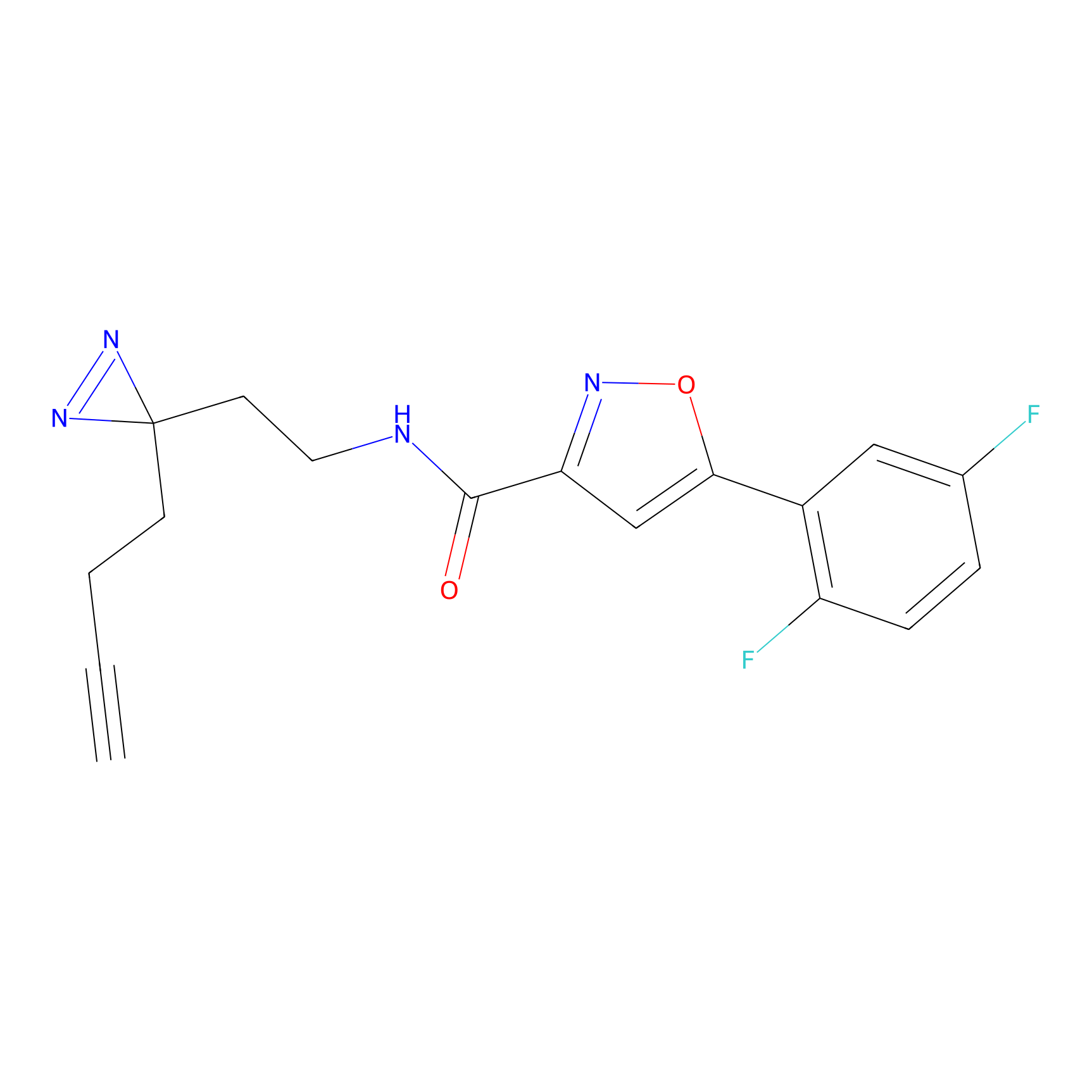
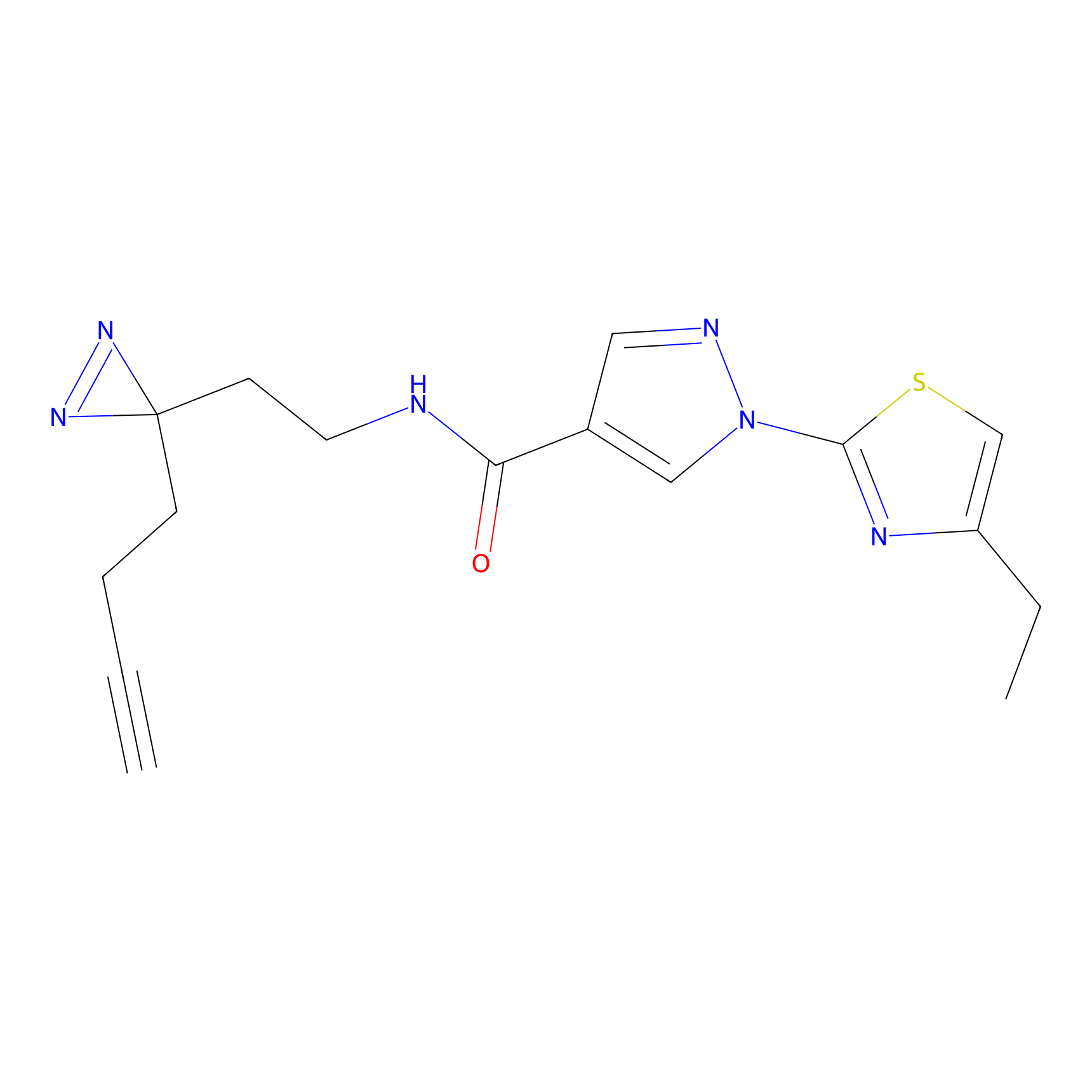
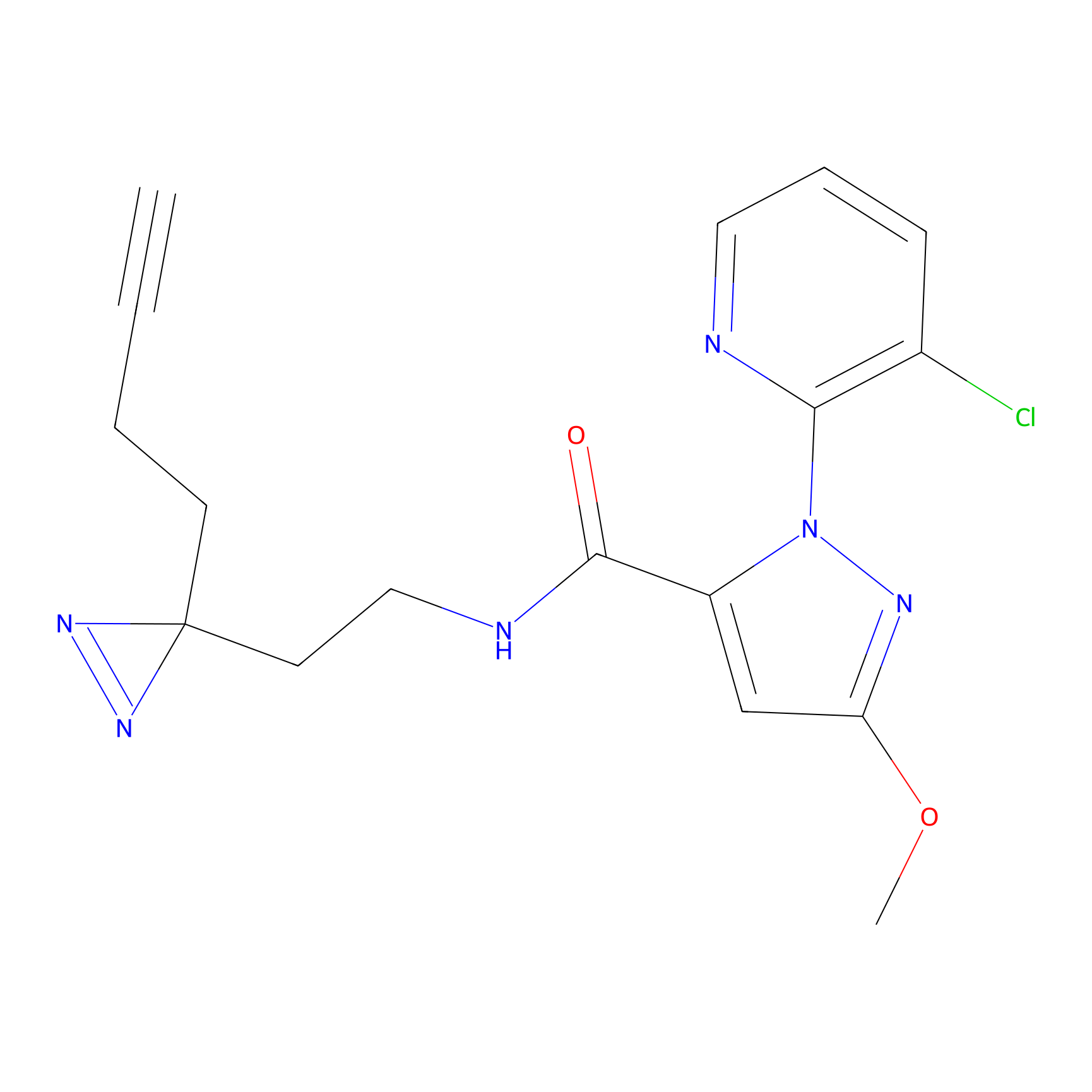
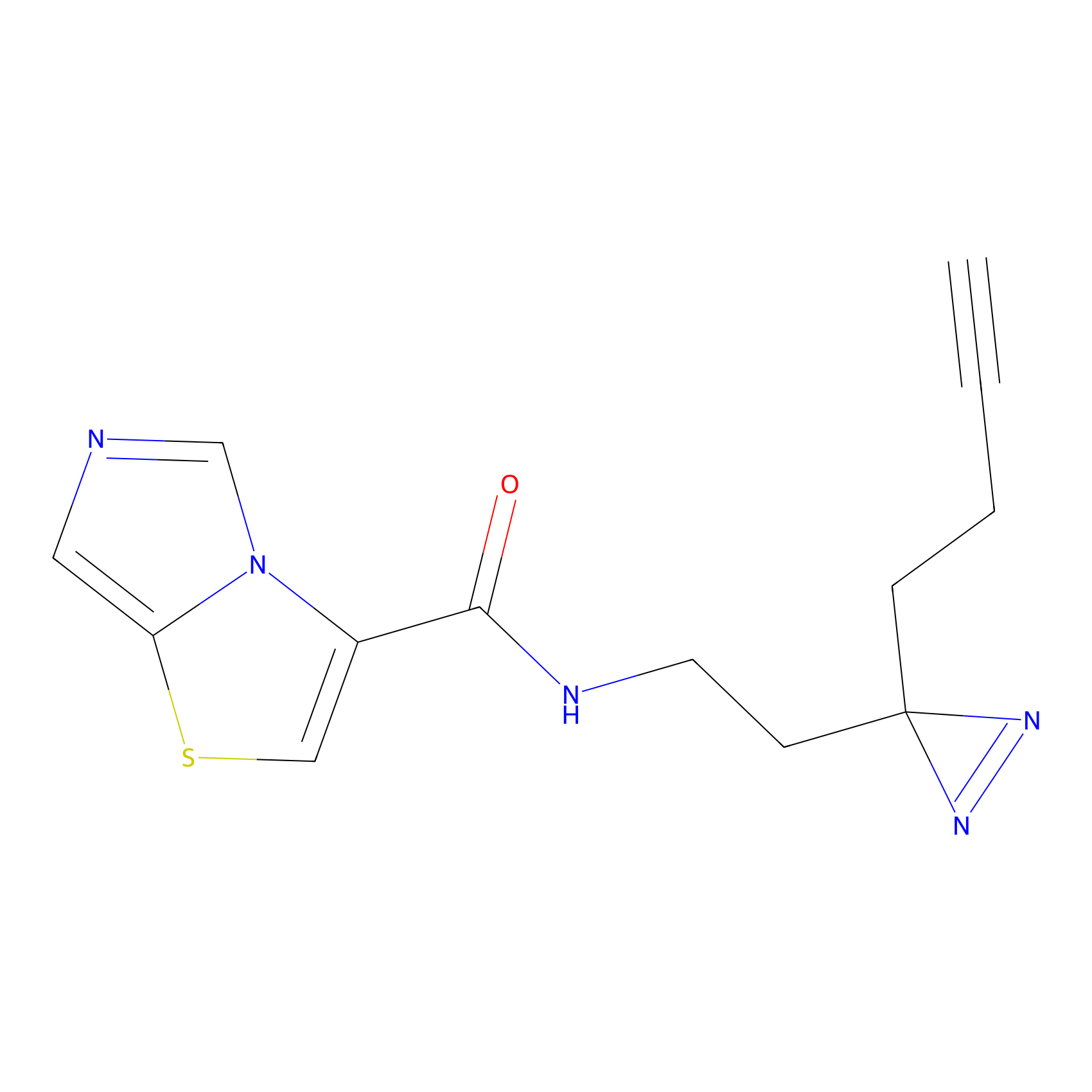
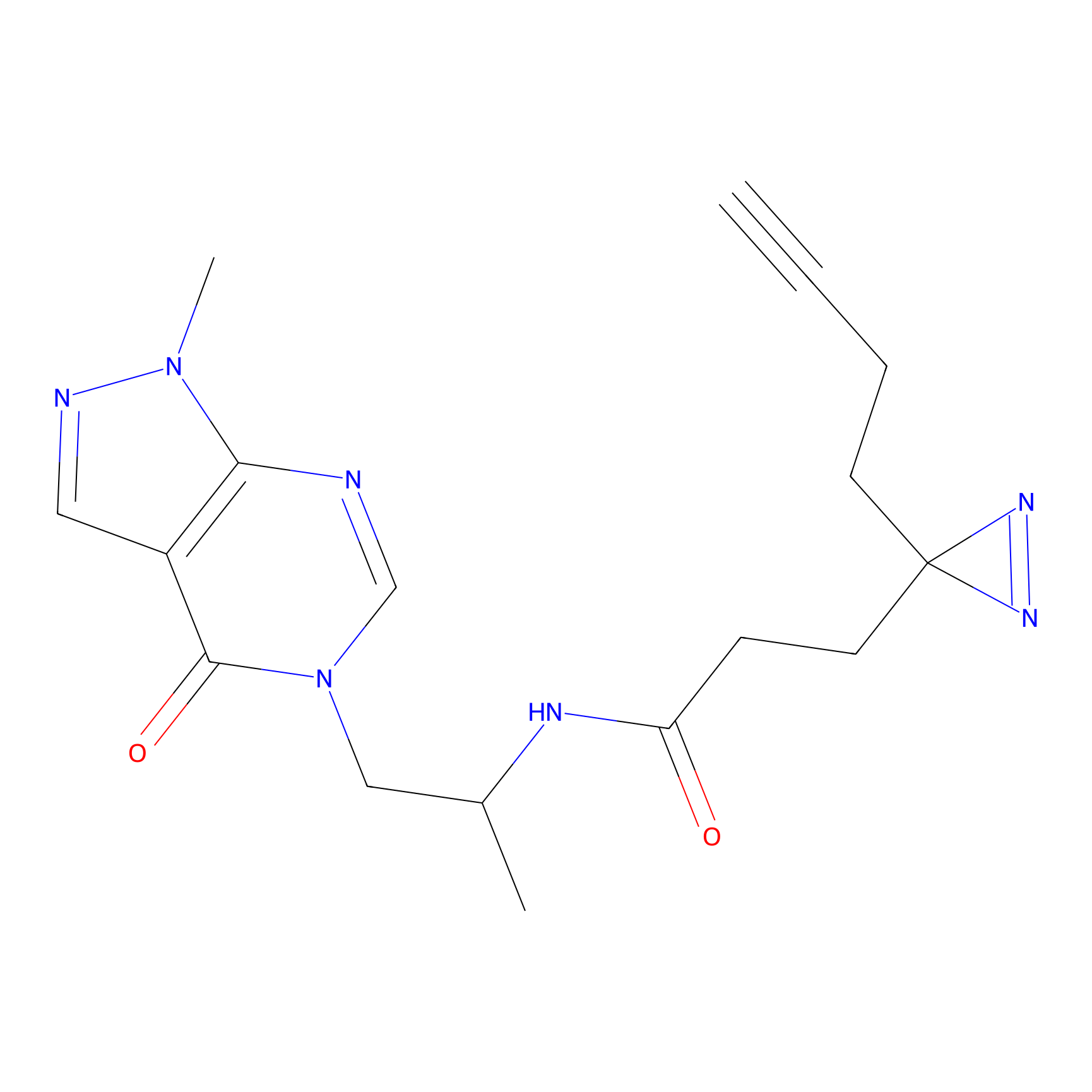
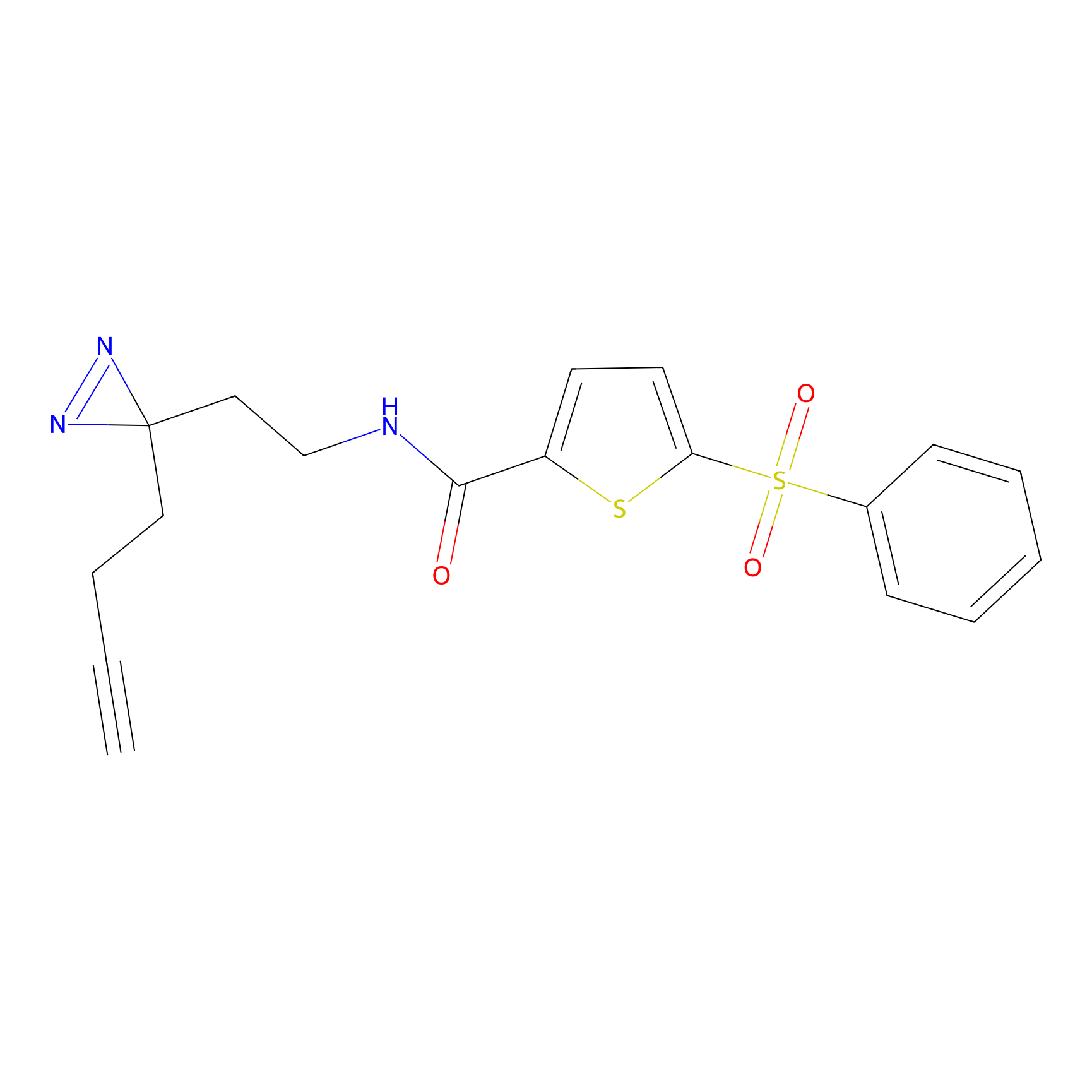
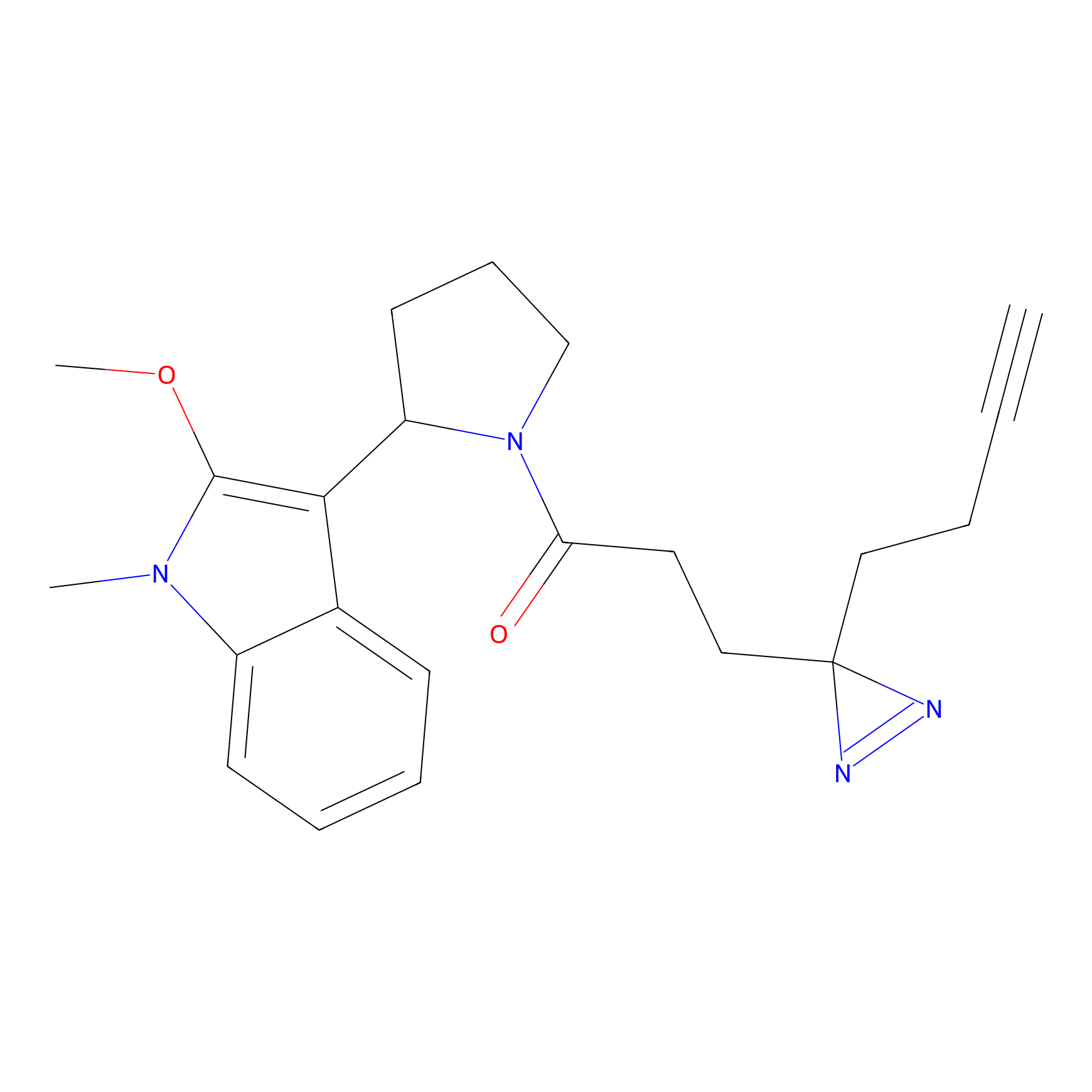
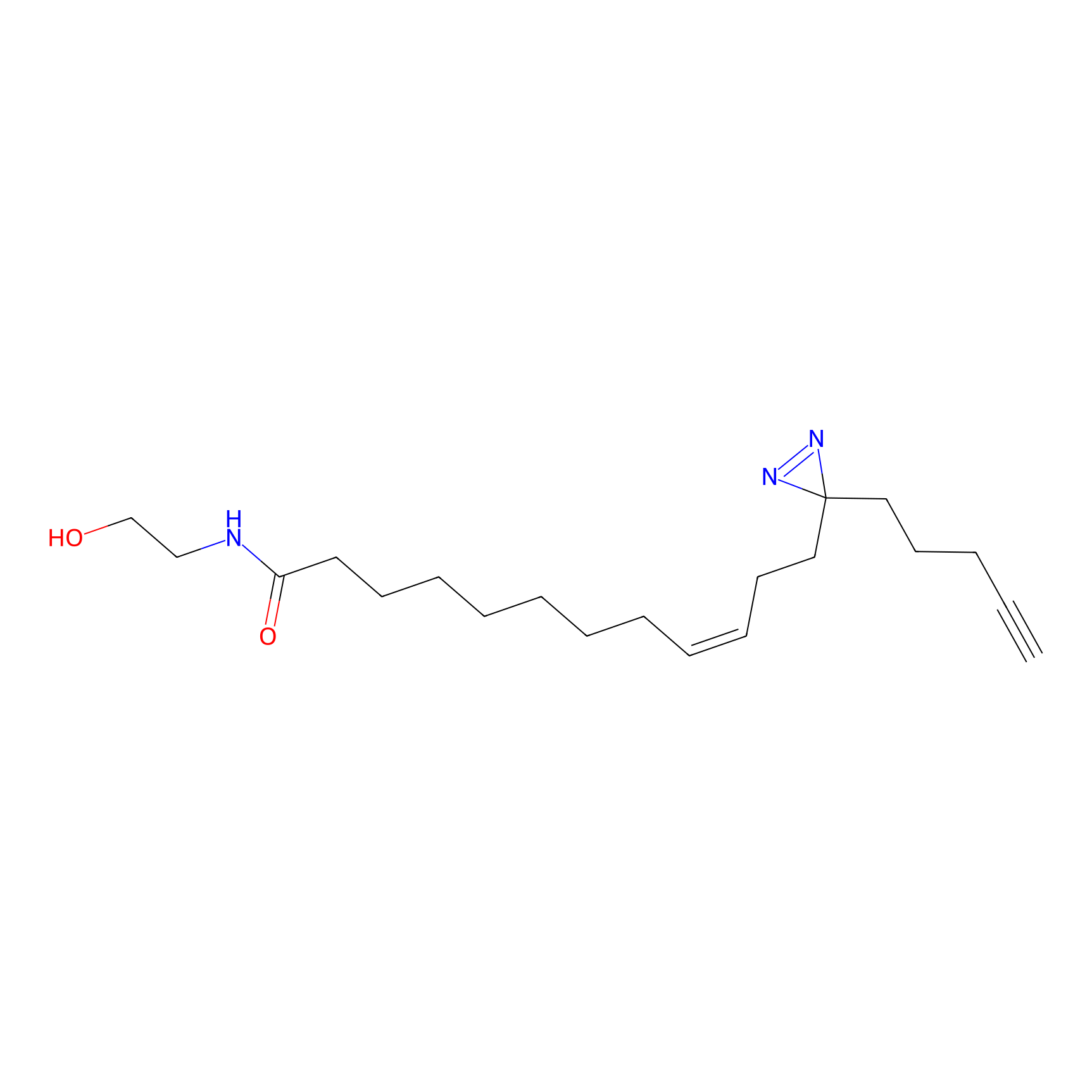
m-APA Probe Info |
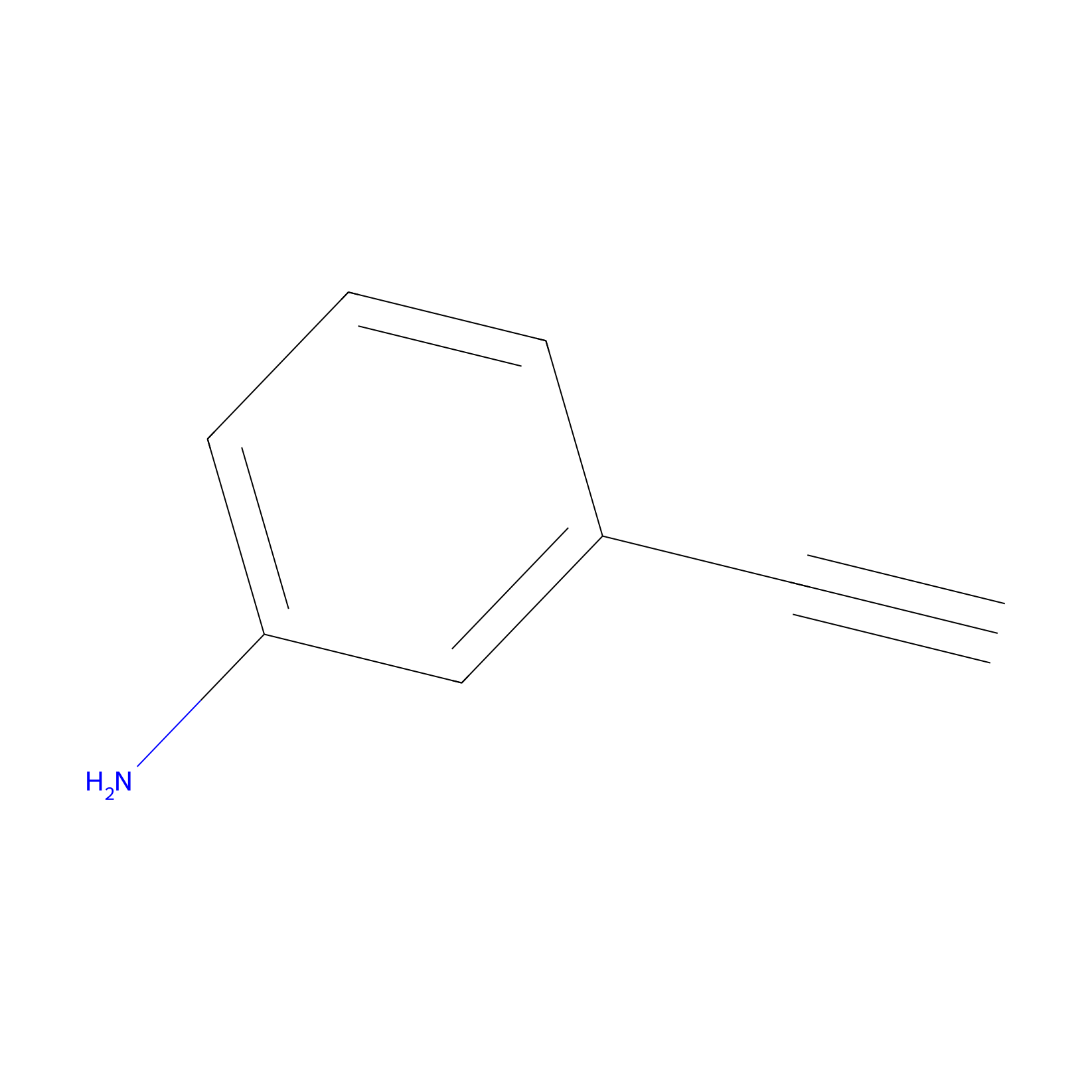 |
N.A. | LDD2231 | [3] | |
|
TFBX Probe Info |
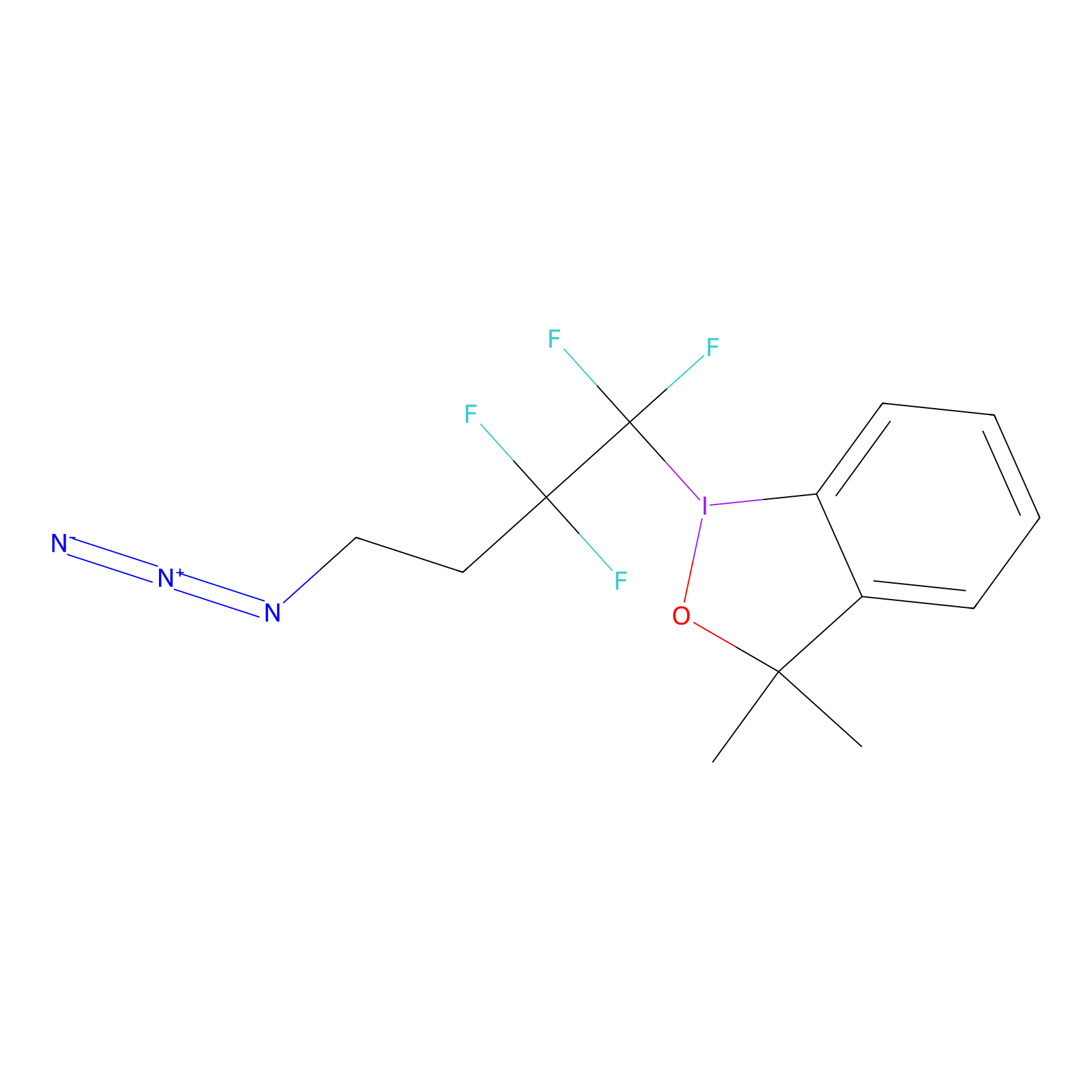 |
N.A. | LDD0027 | [4] | |
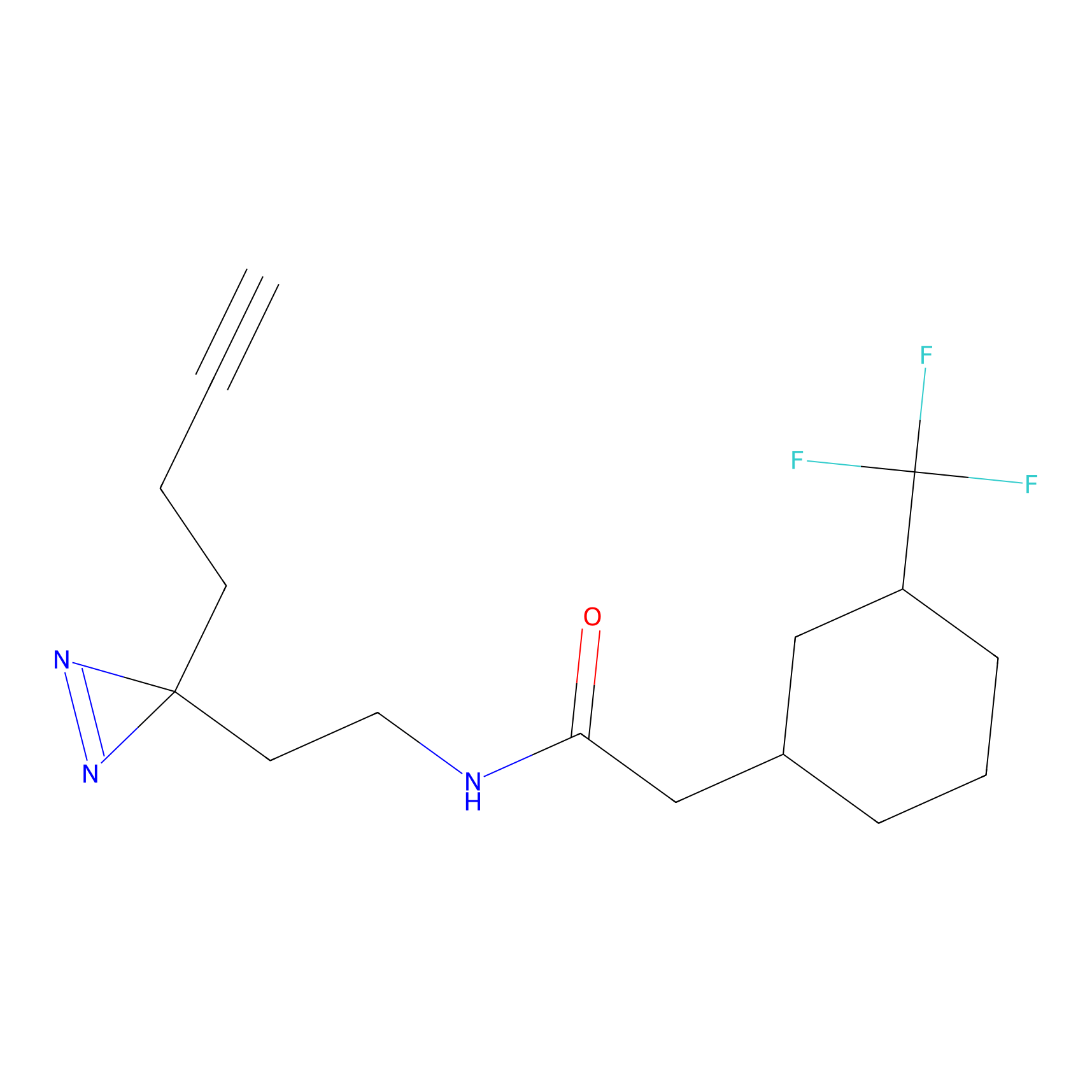
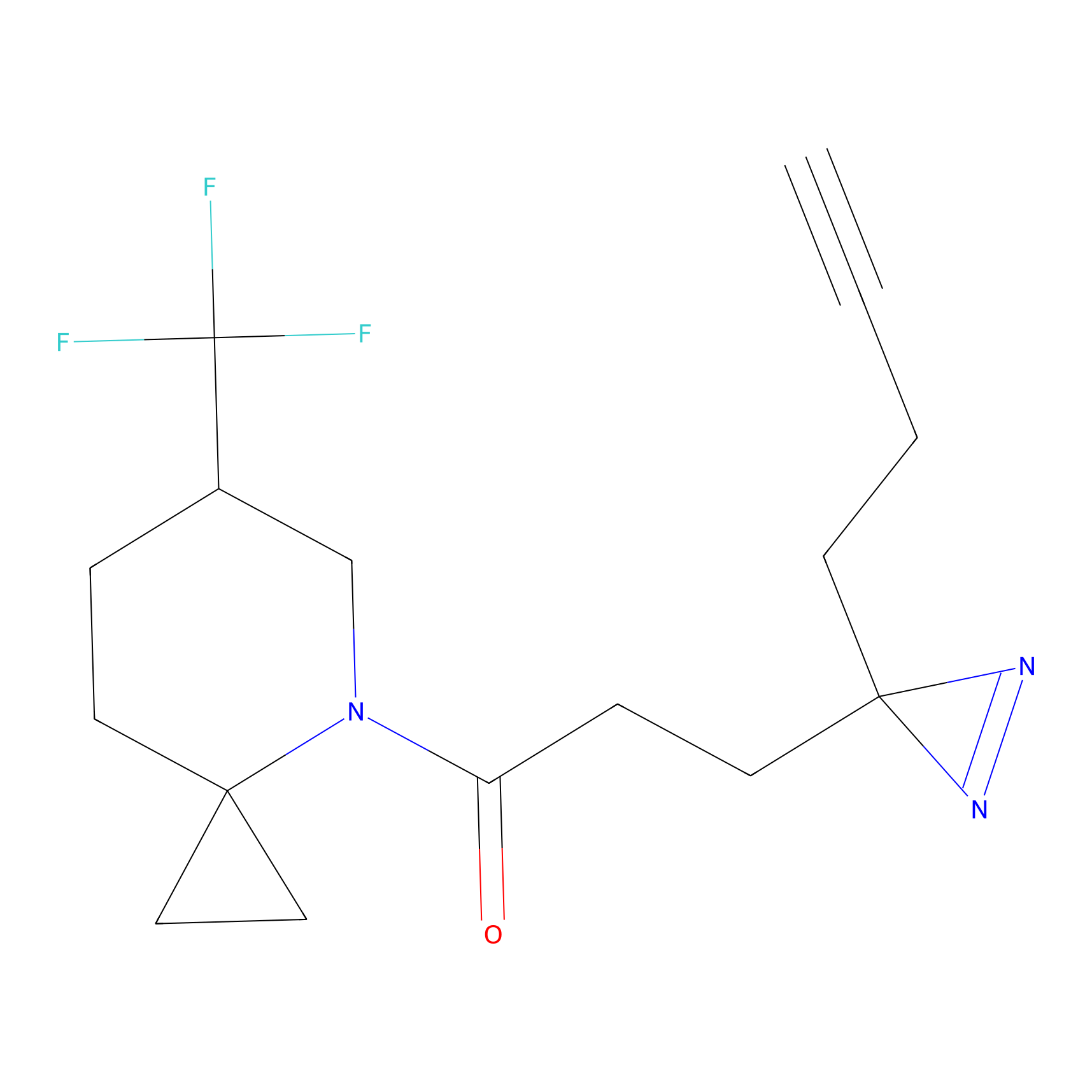
|
IPM Probe Info |
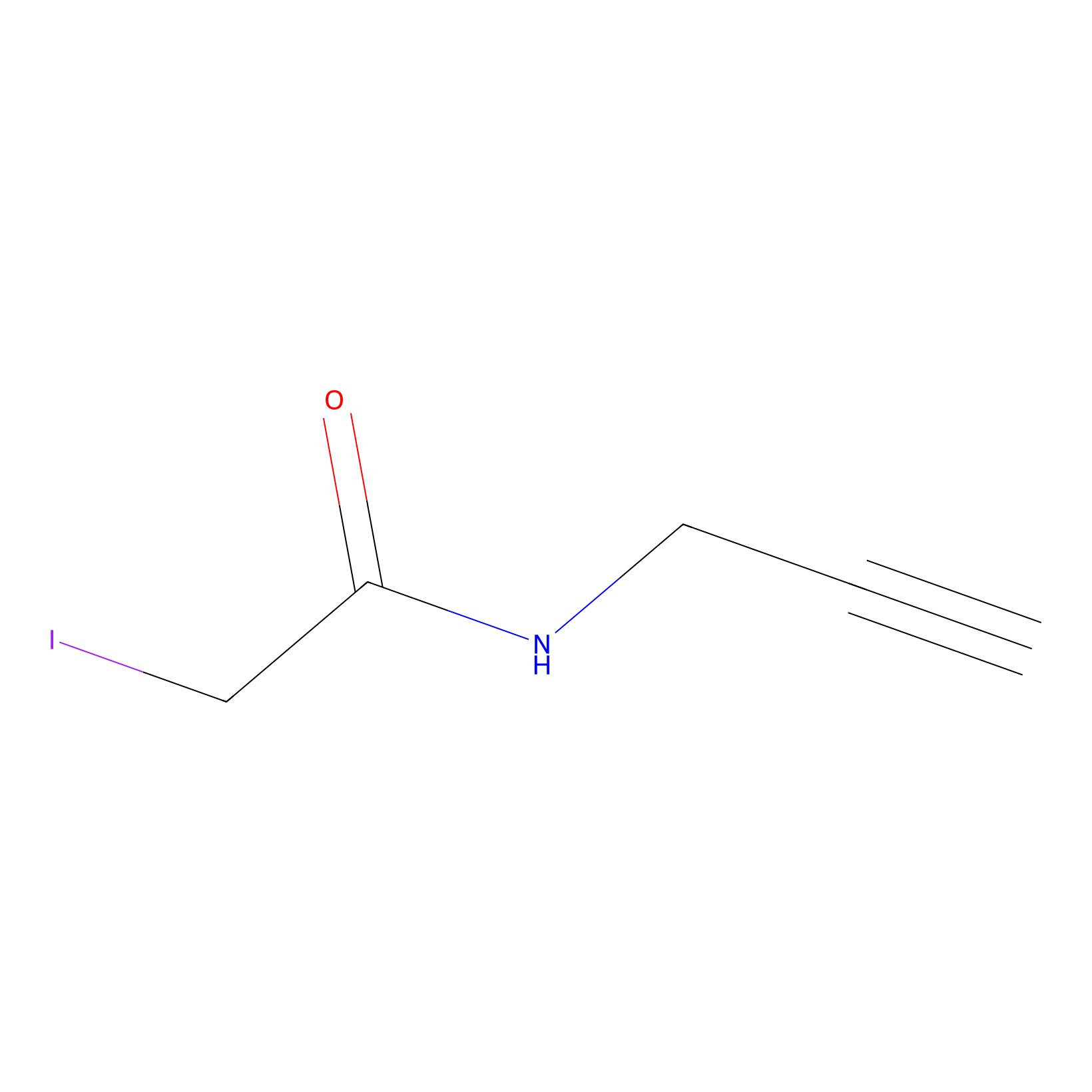 |
N.A. | LDD2156 | [5] | |
|
AOyne Probe Info |
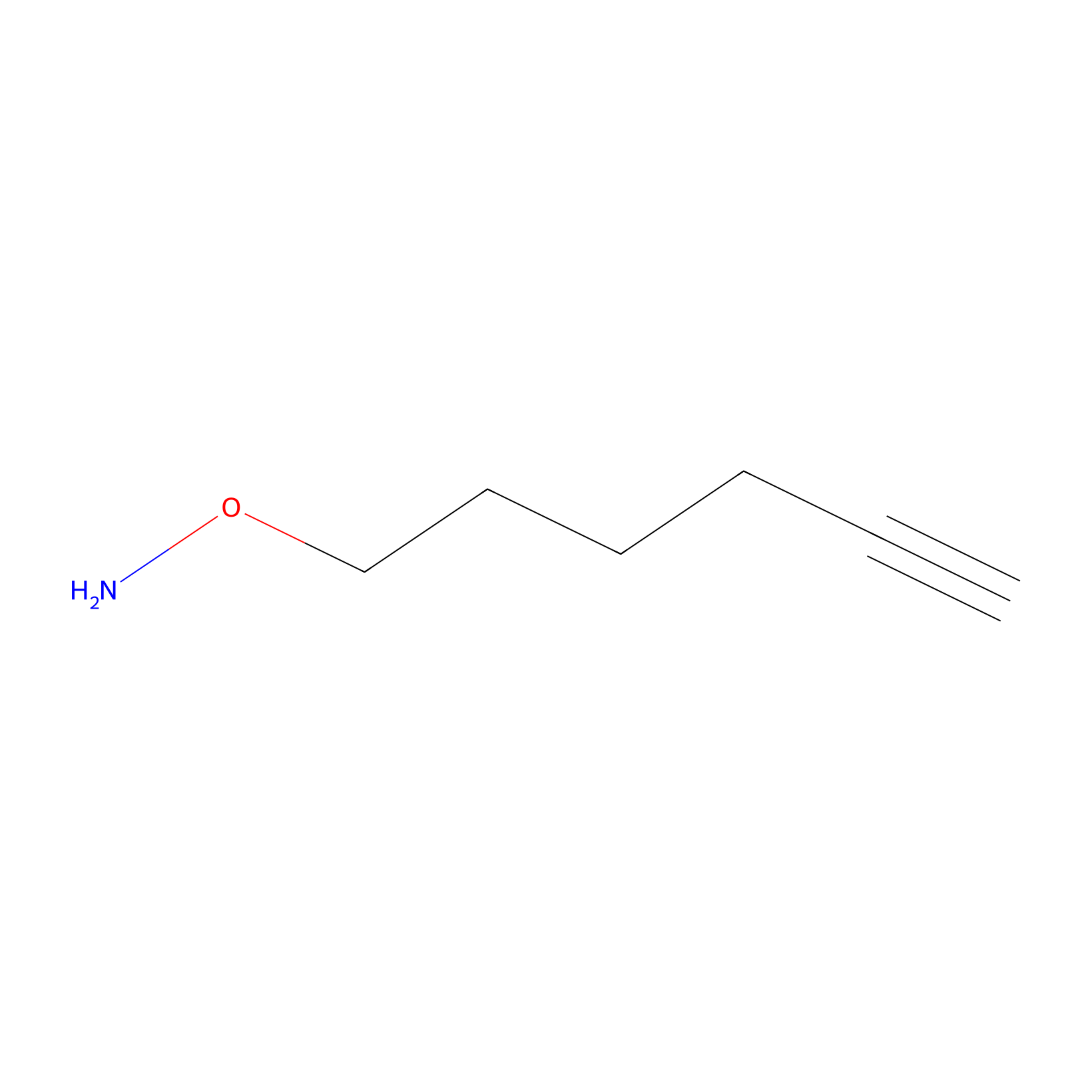 |
15.00 | LDD0443 | [6] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
References