Details of the Target
General Information of Target
| Target ID | LDTP06097 | |||||
|---|---|---|---|---|---|---|
| Target Name | Reticulocalbin-2 (RCN2) | |||||
| Gene Name | RCN2 | |||||
| Gene ID | 5955 | |||||
| Synonyms |
ERC55; Reticulocalbin-2; Calcium-binding protein ERC-55; E6-binding protein; E6BP |
|||||
| 3D Structure | ||||||
| Sequence |
MRLGPRTAALGLLLLCAAAAGAGKAEELHYPLGERRSDYDREALLGVQEDVDEYVKLGHE
EQQKRLQAIIKKIDLDSDGFLTESELSSWIQMSFKHYAMQEAKQQFVEYDKNSDDTVTWD EYNIQMYDRVIDFDENTALDDAEEESFRKLHLKDKKRFEKANQDSGPGLSLEEFIAFEHP EEVDYMTEFVIQEALEEHDKNGDGFVSLEEFLGDYRWDPTANEDPEWILVEKDRFVNDYD KDNDGRLDPQELLPWVVPNNQGIAQEEALHLIDEMDLNGDKKLSEEEILENPDLFLTSEA TDYGRQLHDDYFYHDEL |
|||||
| Target Bioclass |
Other
|
|||||
| Family |
CREC family
|
|||||
| Subcellular location |
Endoplasmic reticulum lumen
|
|||||
| Function | Not known. Binds calcium. | |||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Target Site Mutations in Different Cell Lines
Probe(s) Labeling This Target
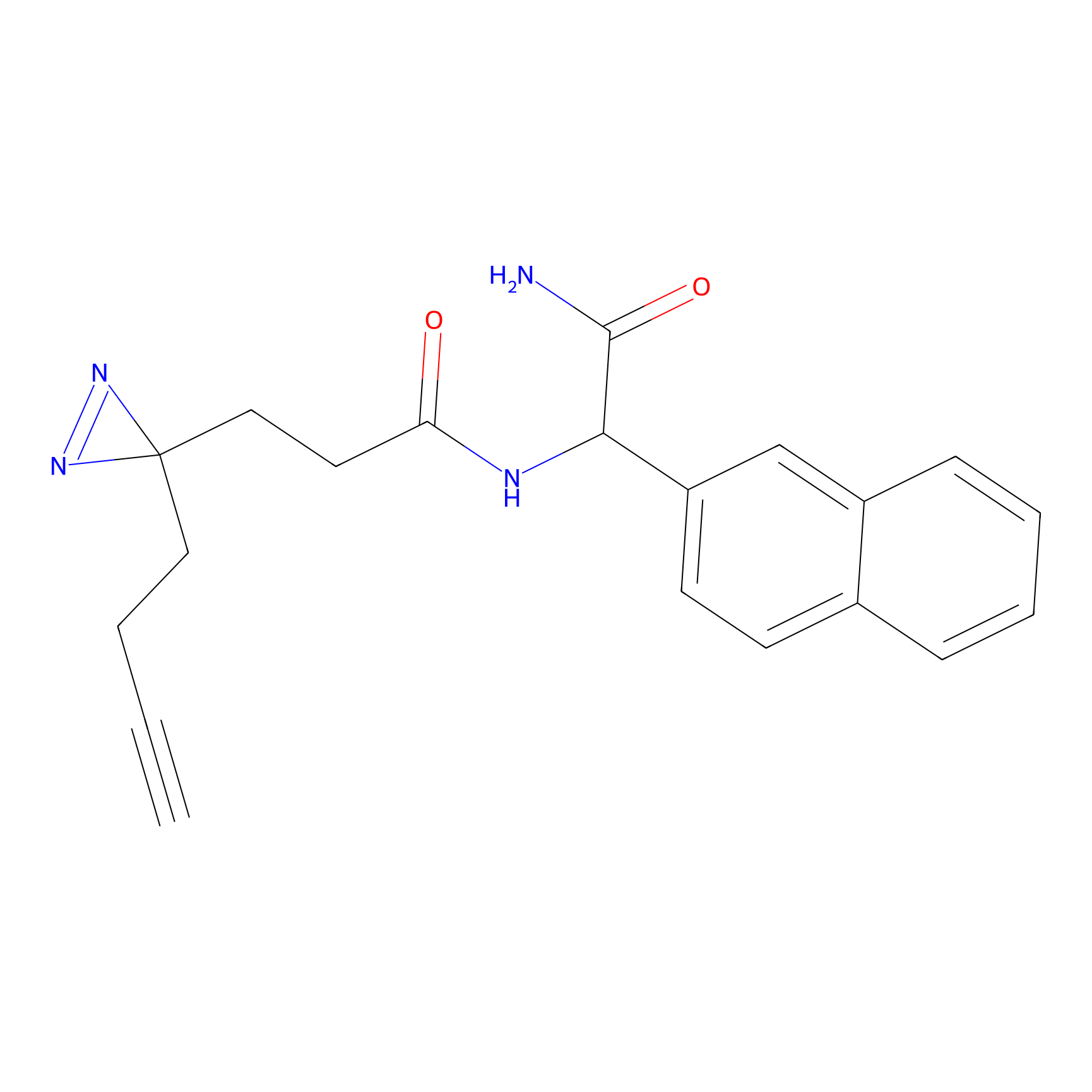
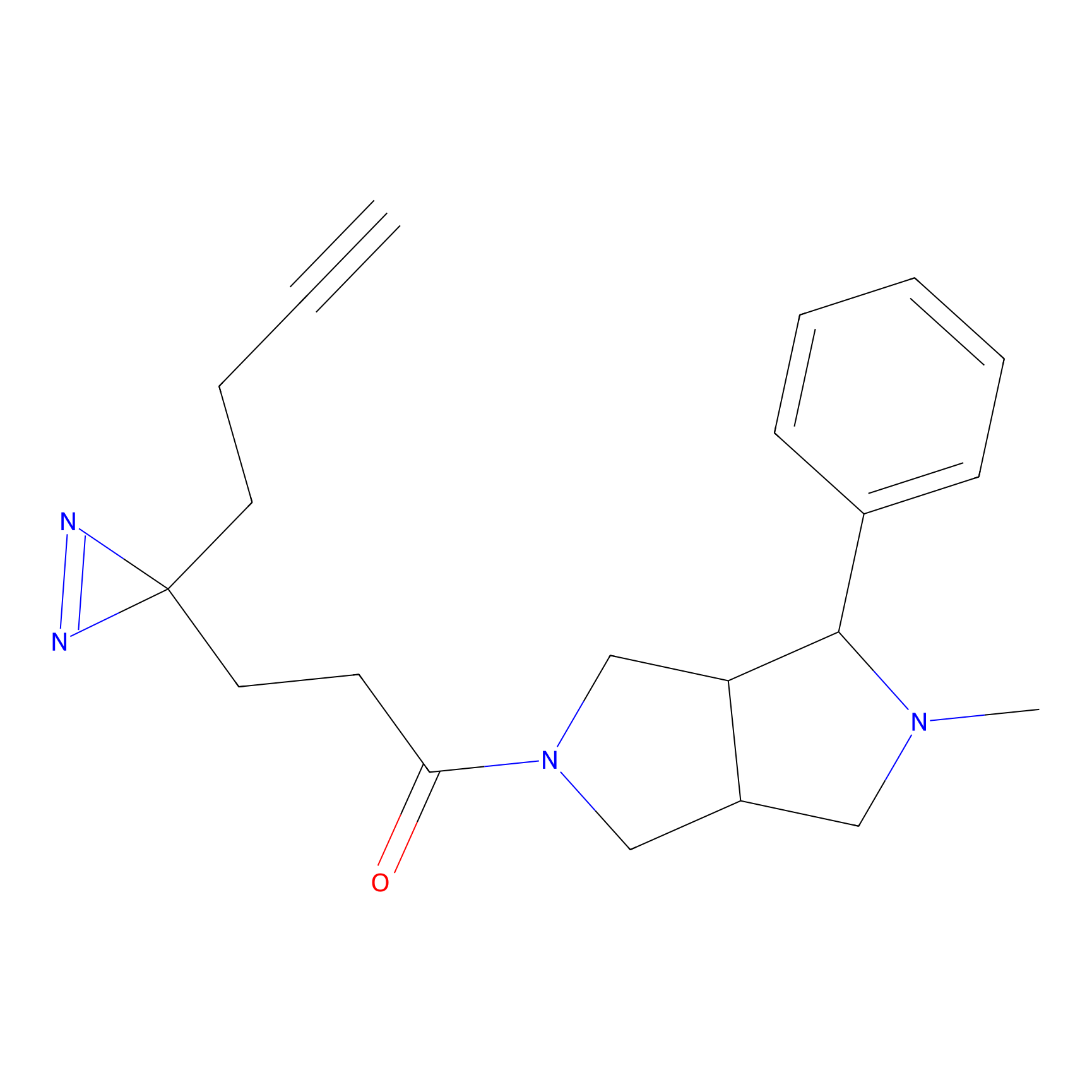
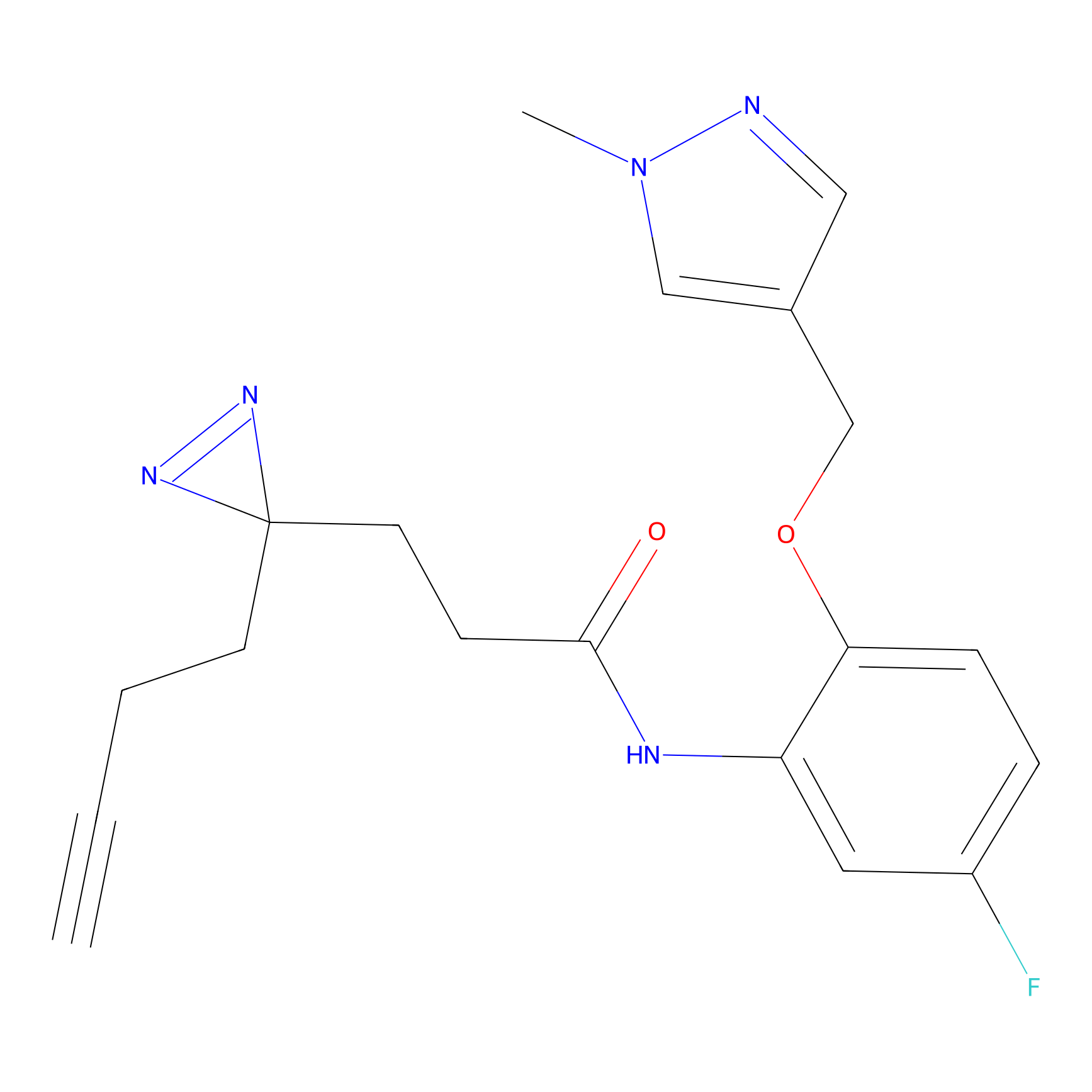
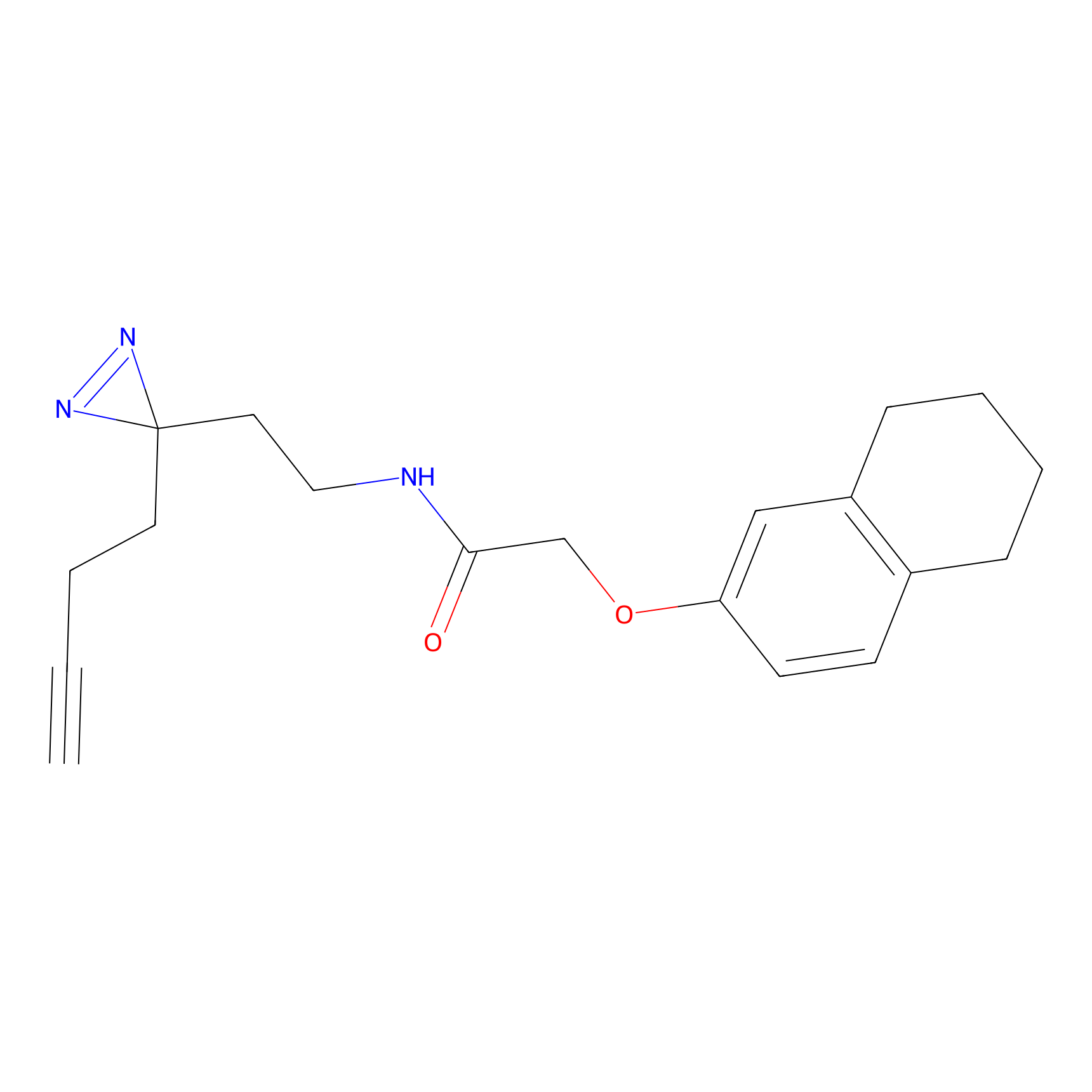
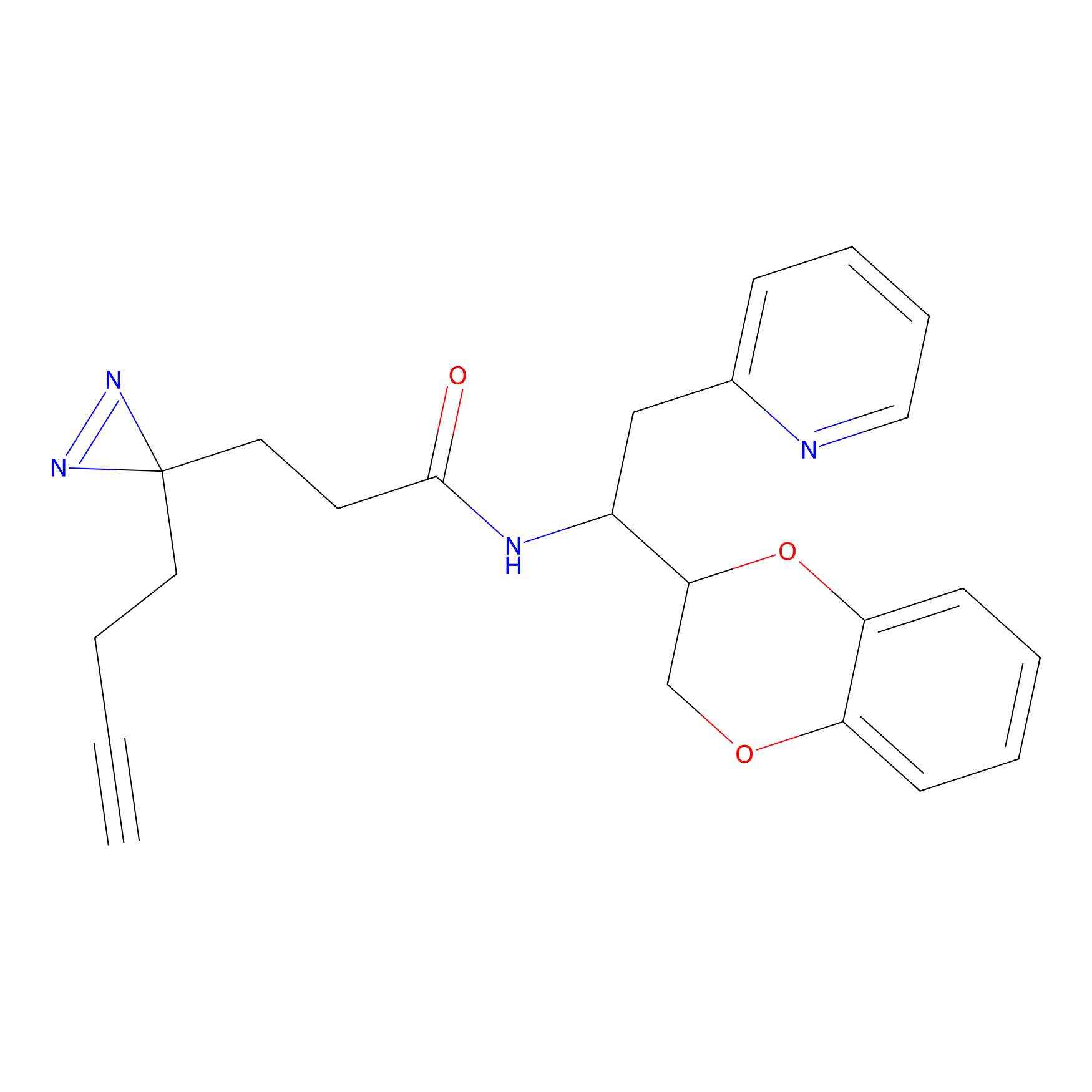
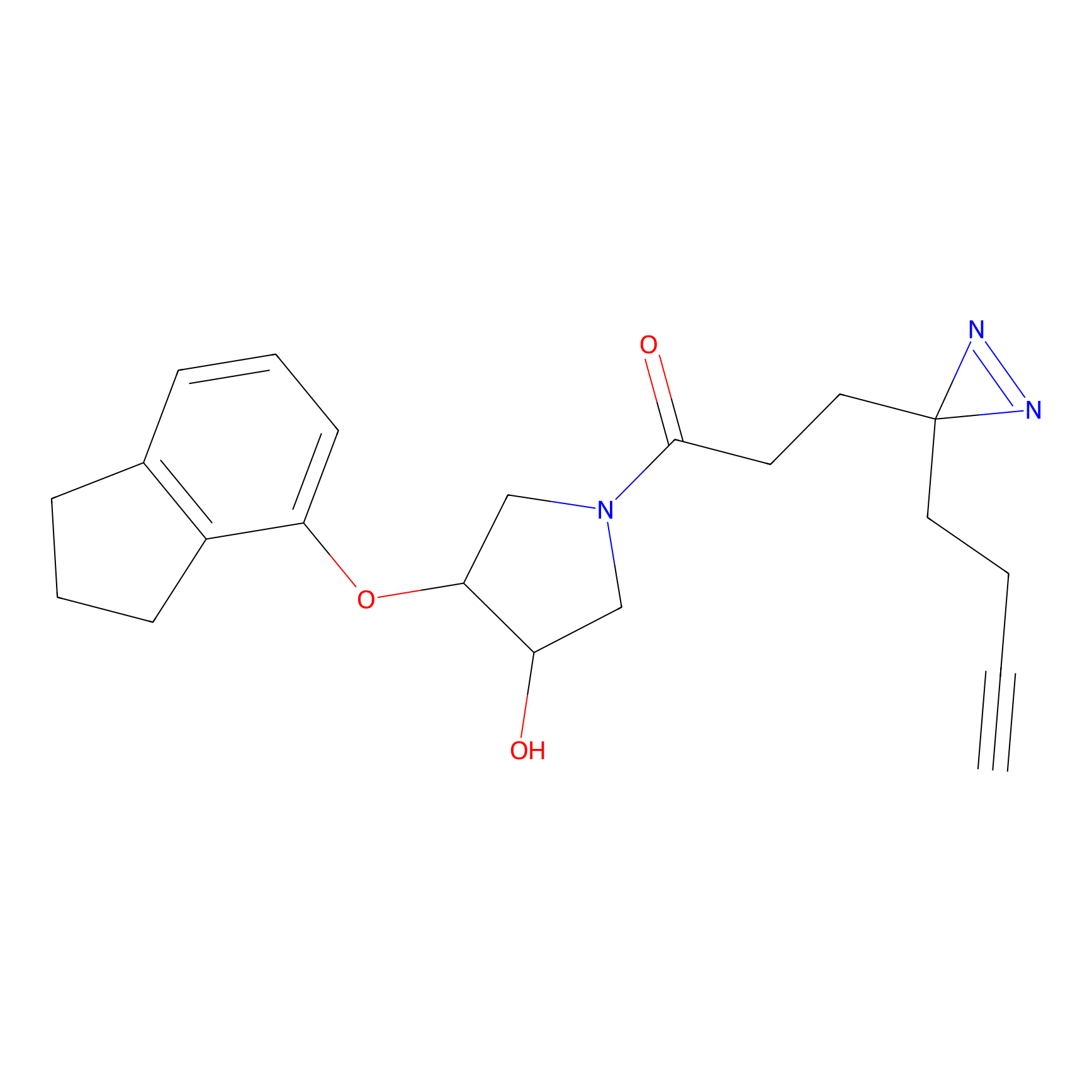
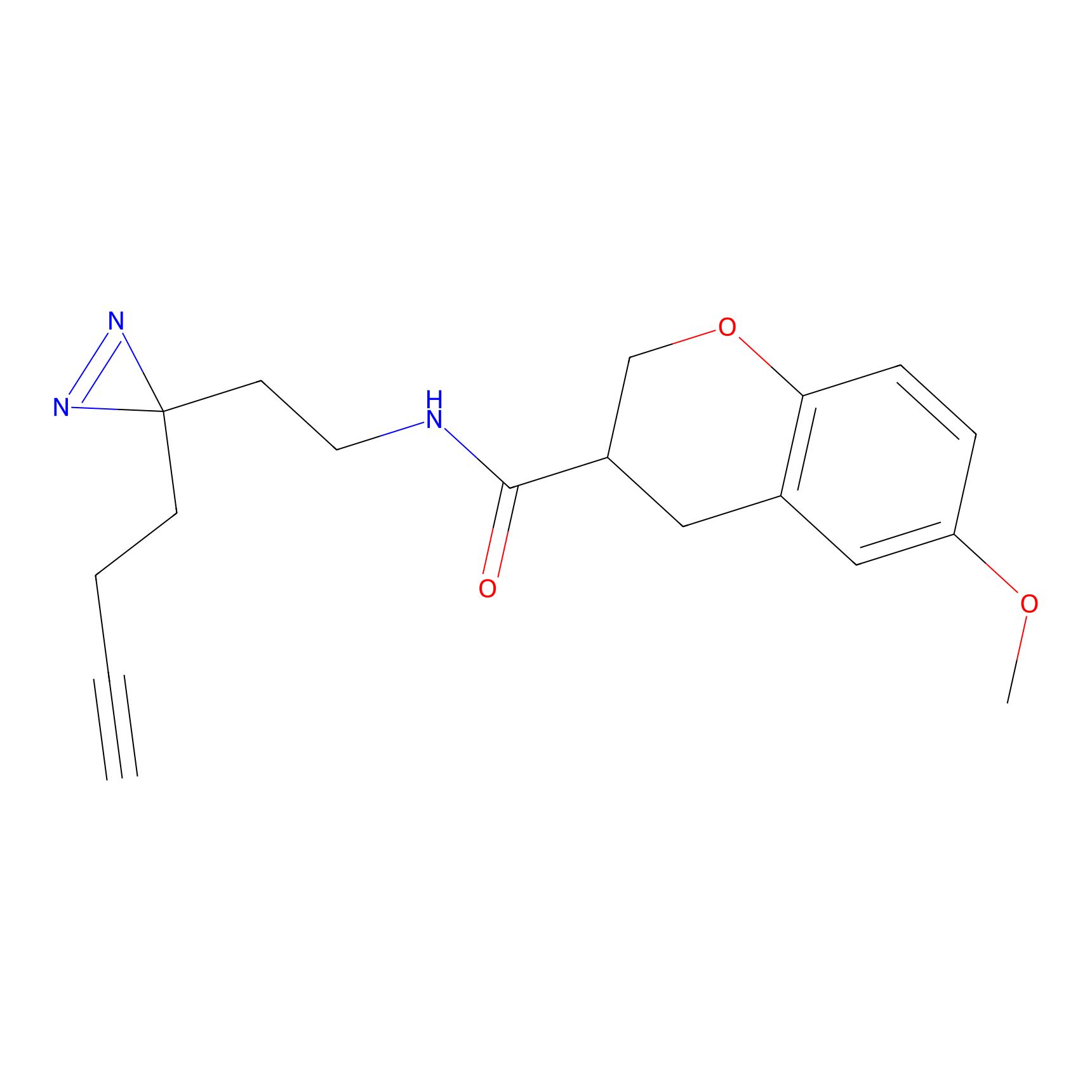
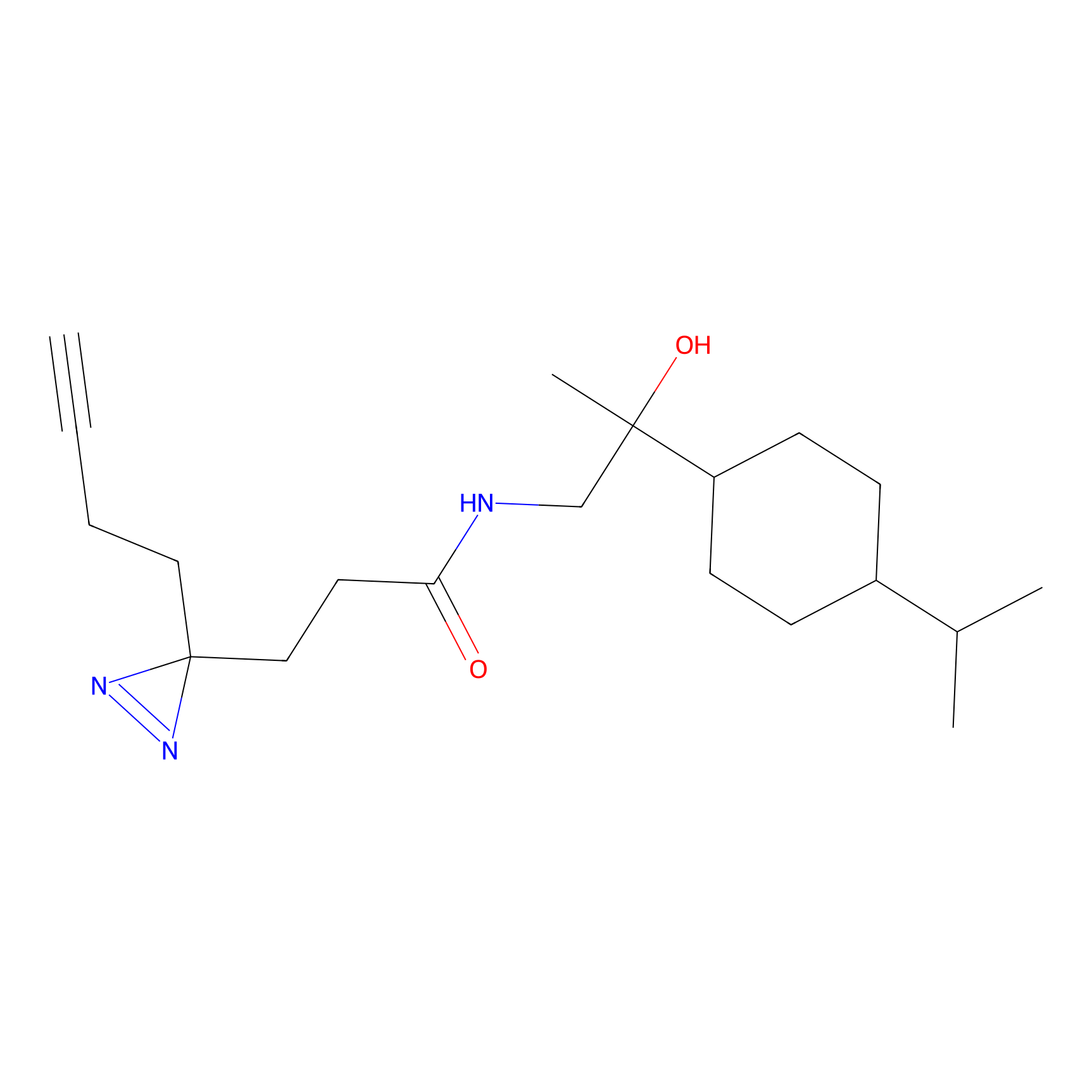
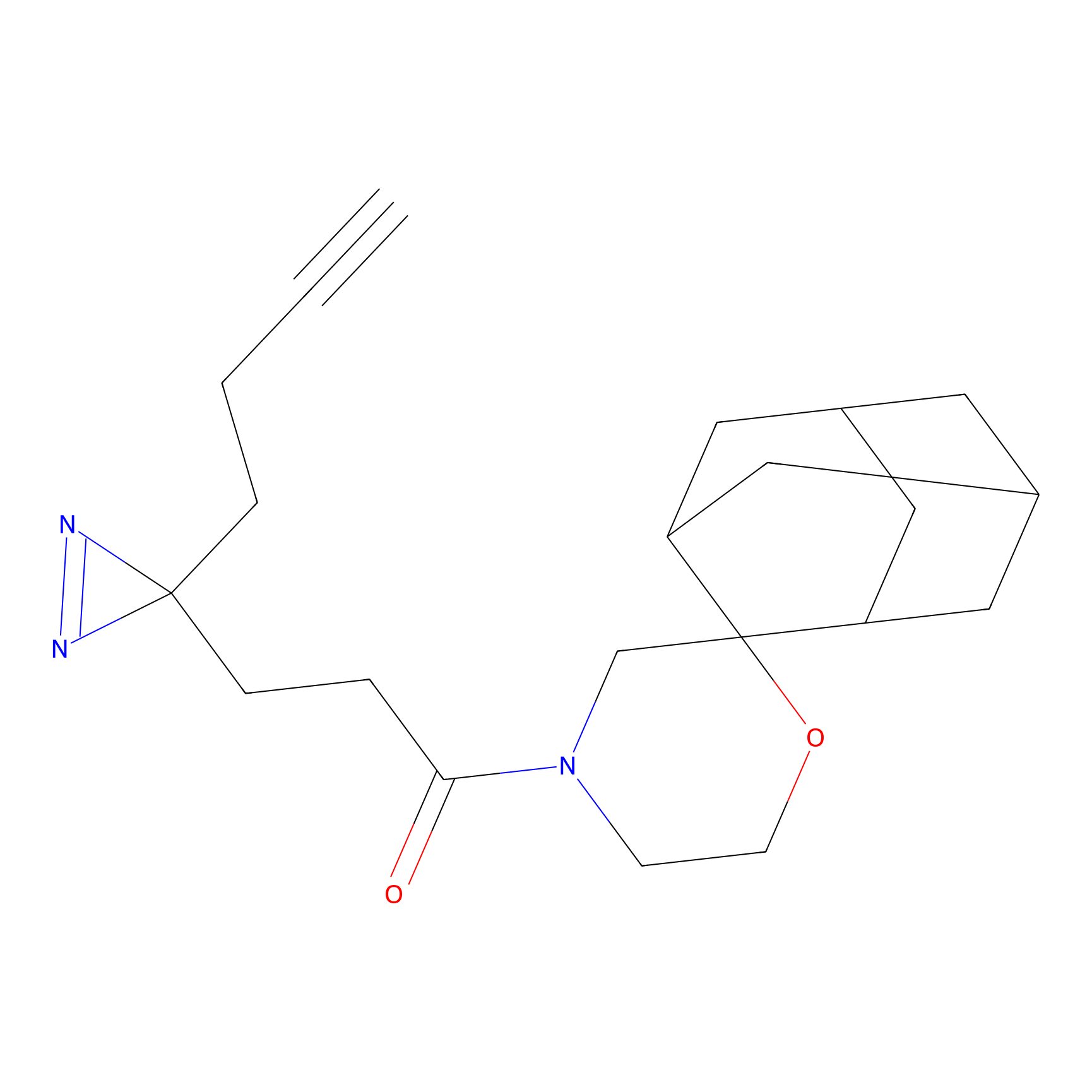
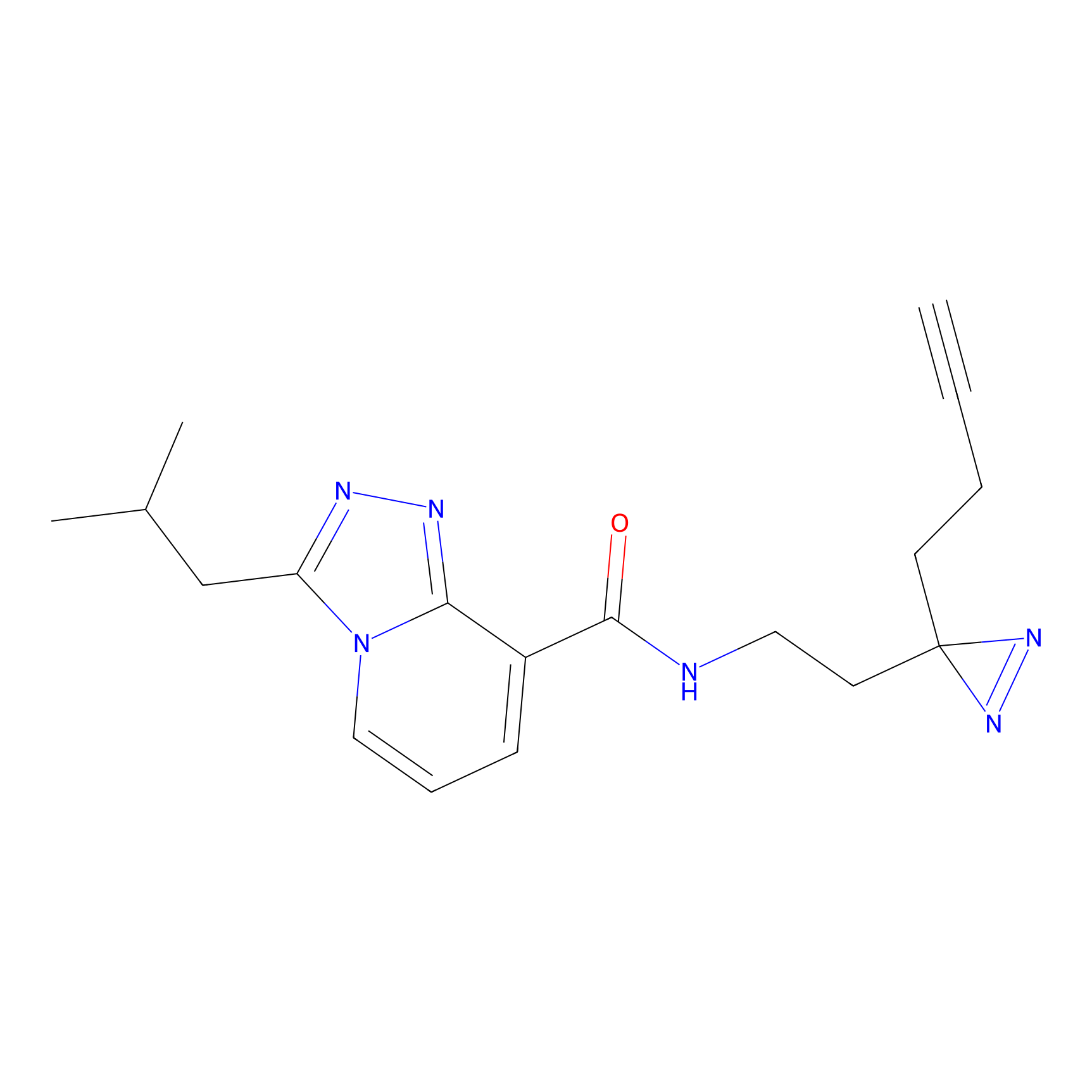
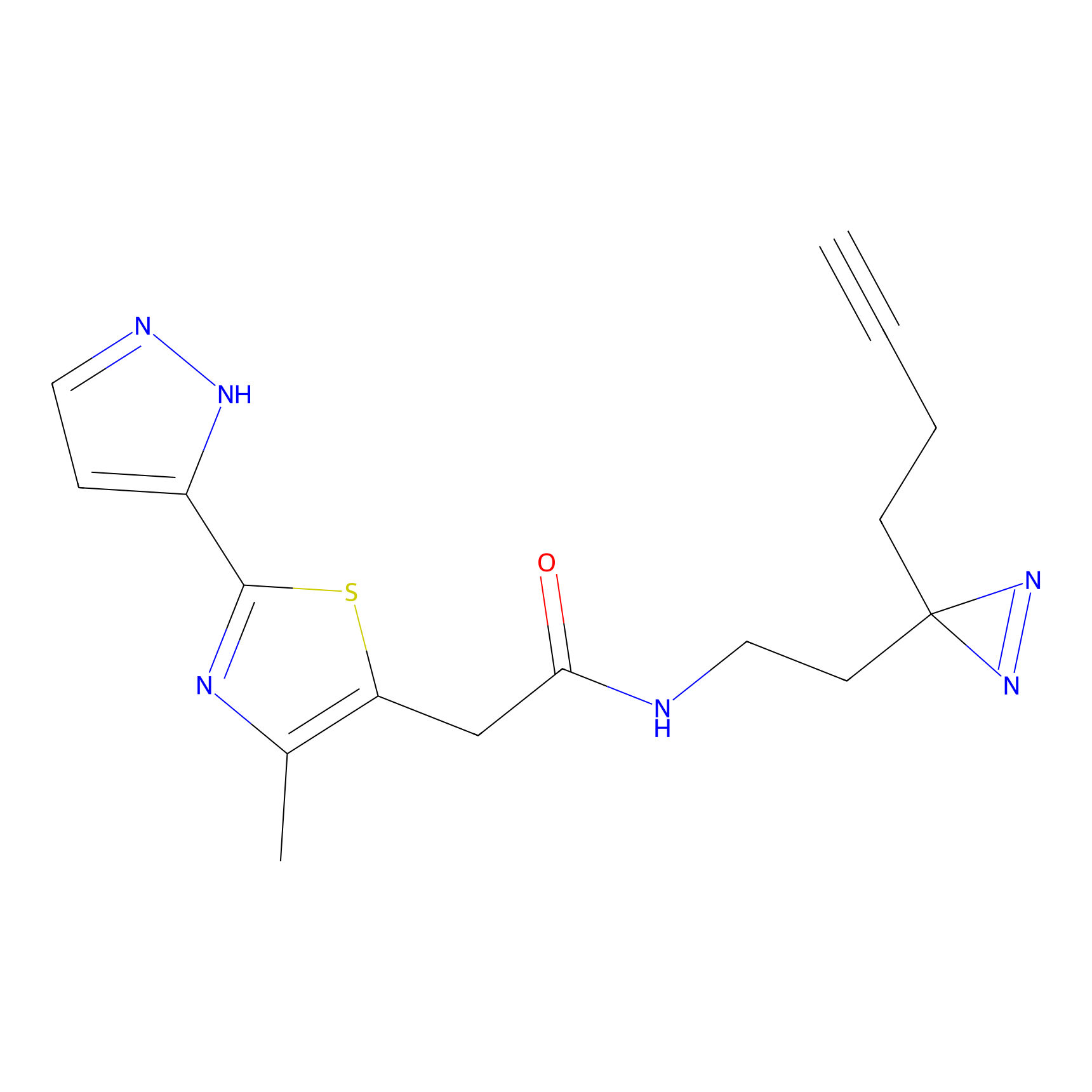
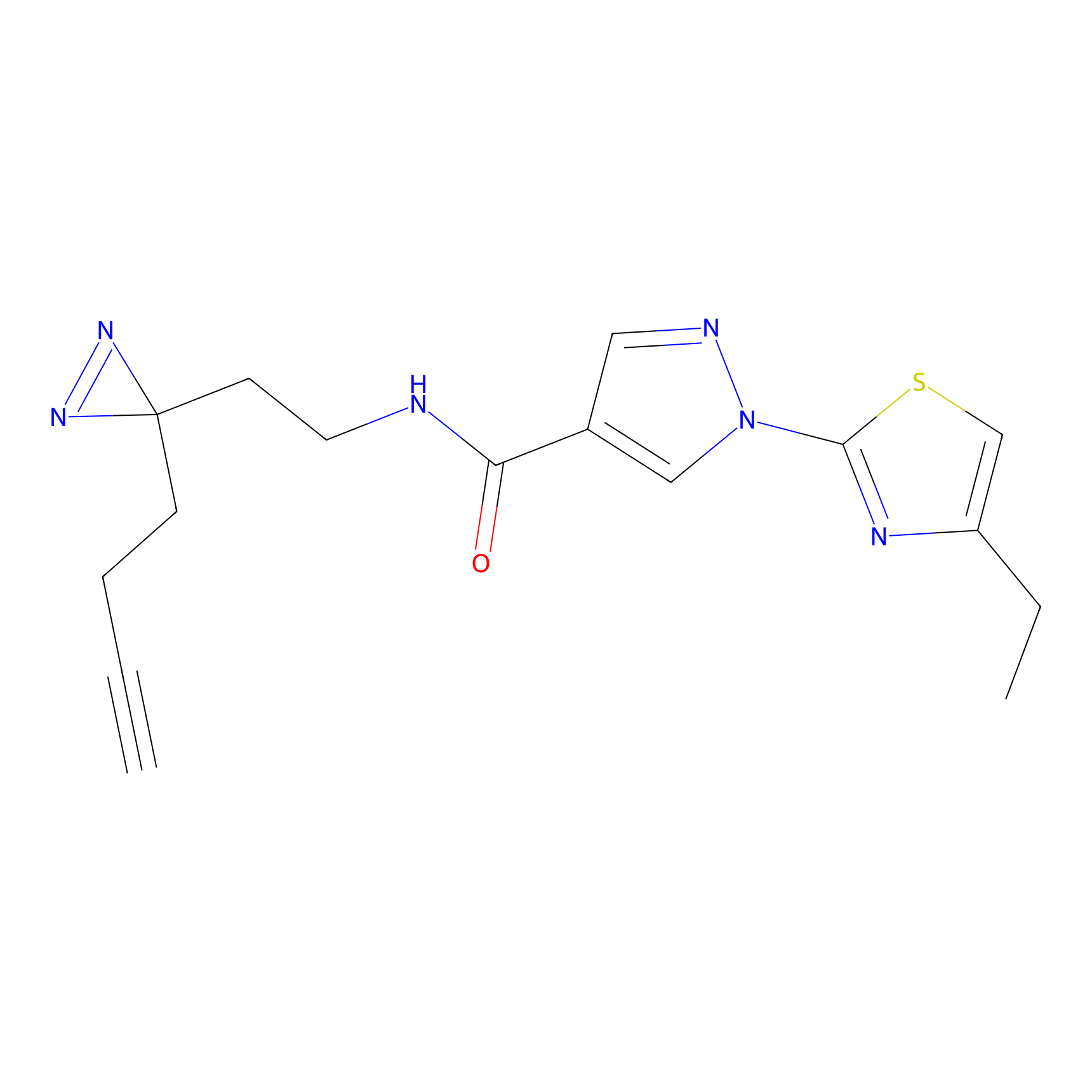
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
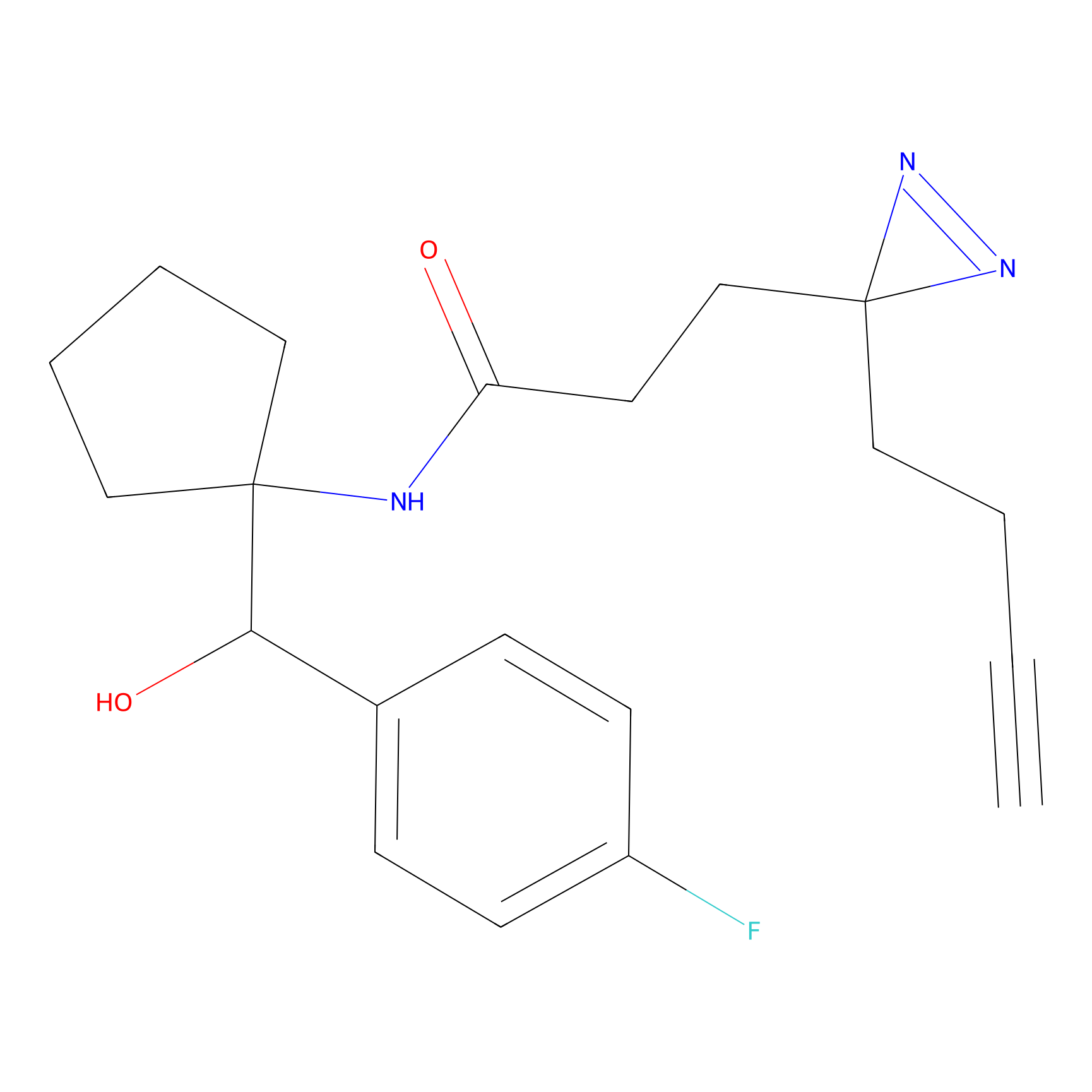
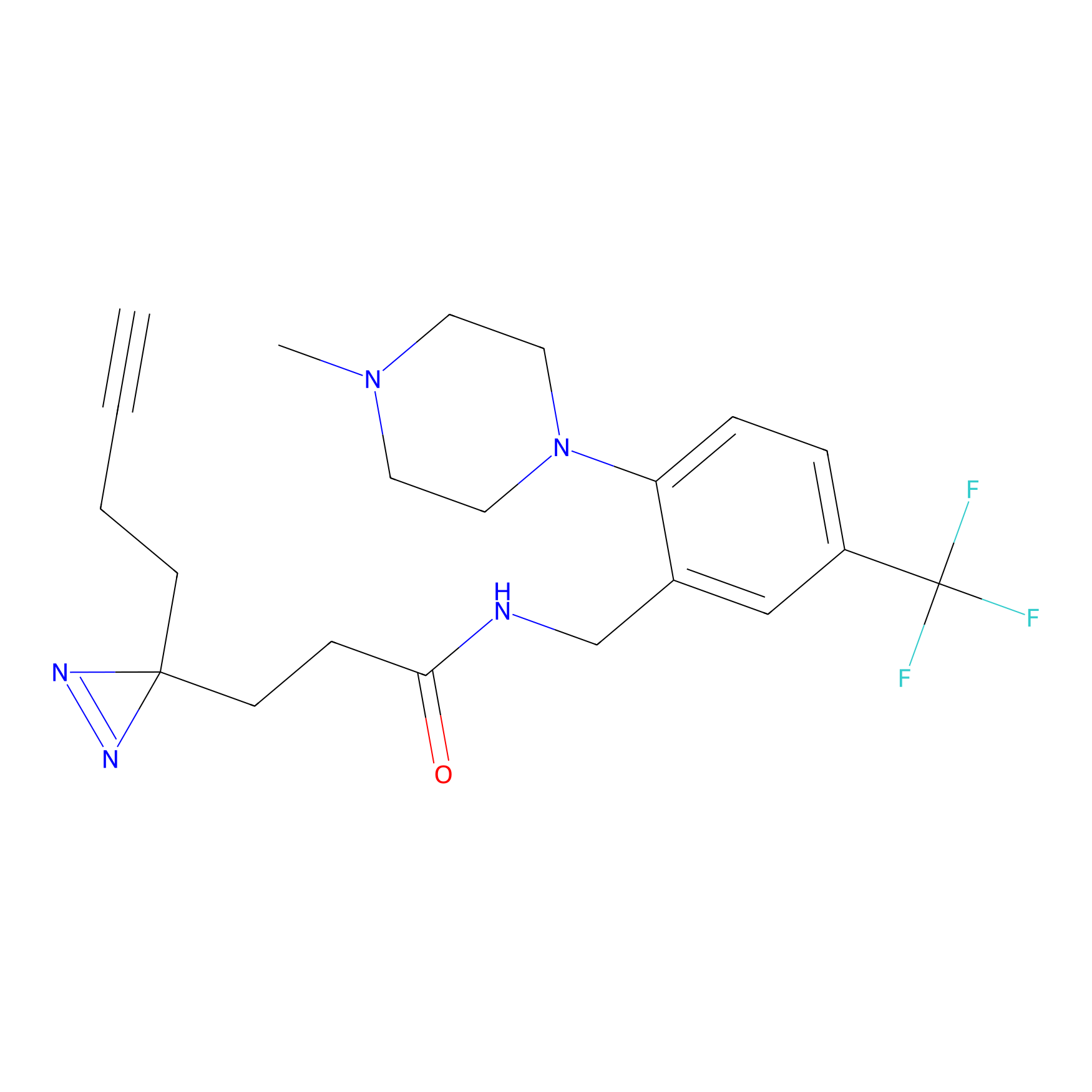
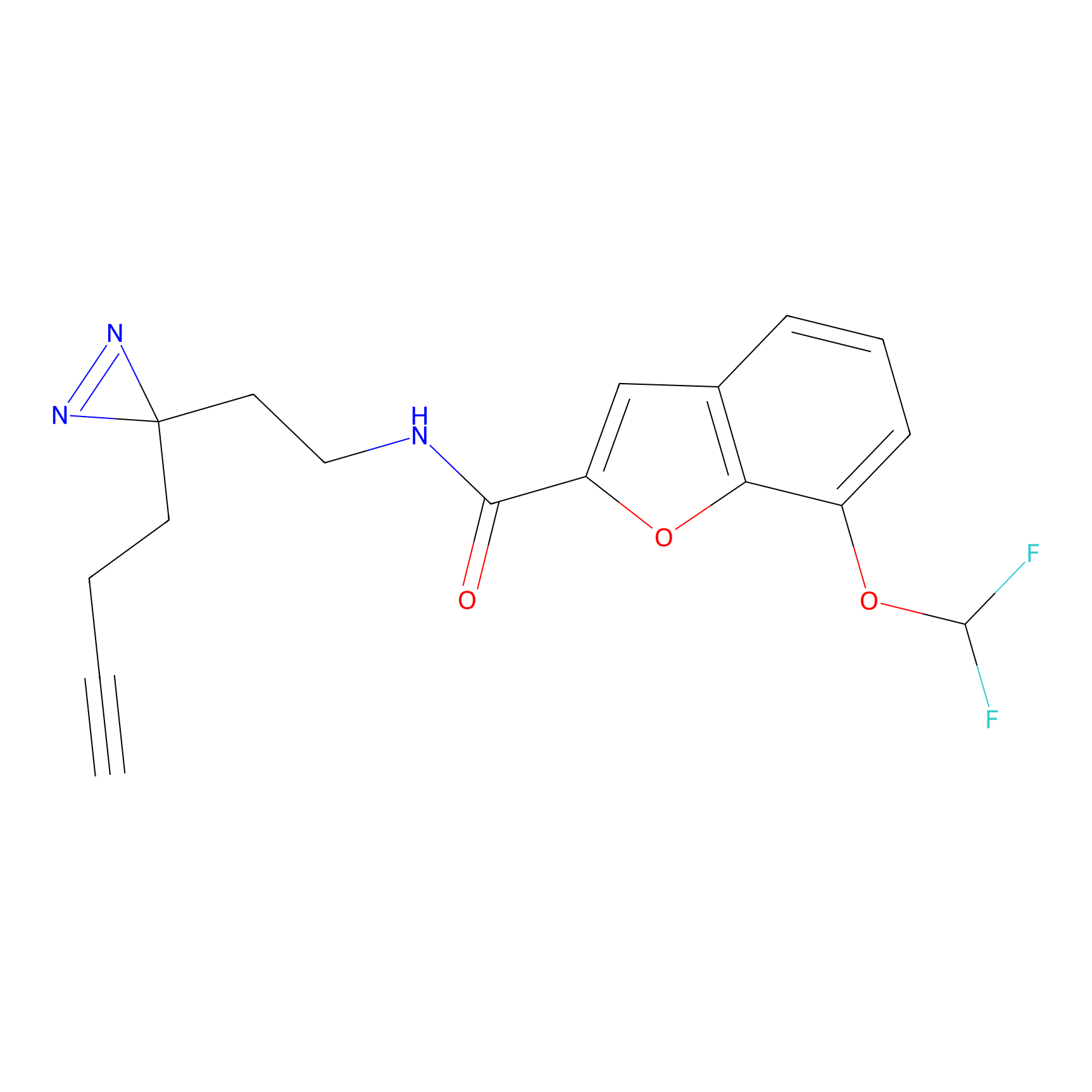
|
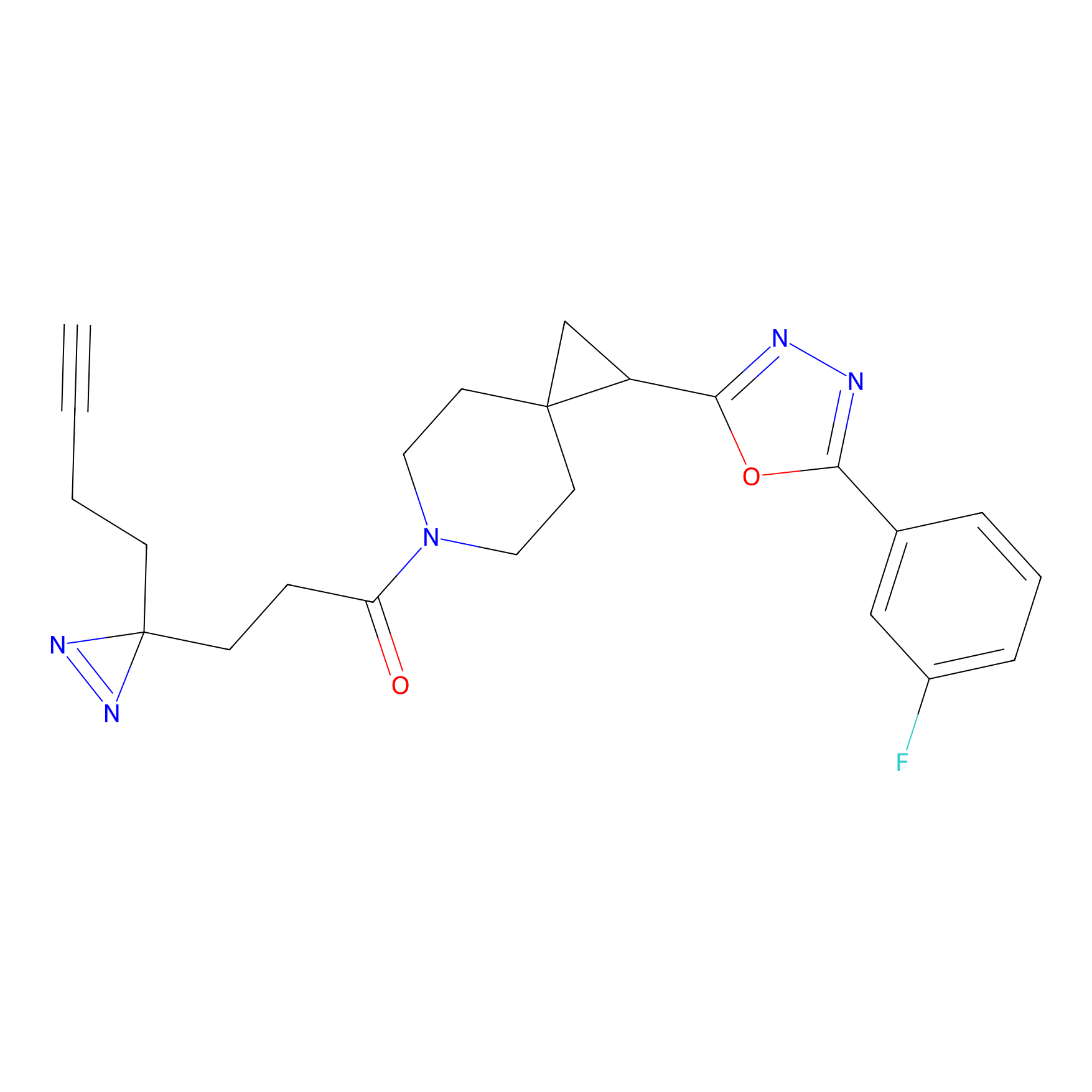
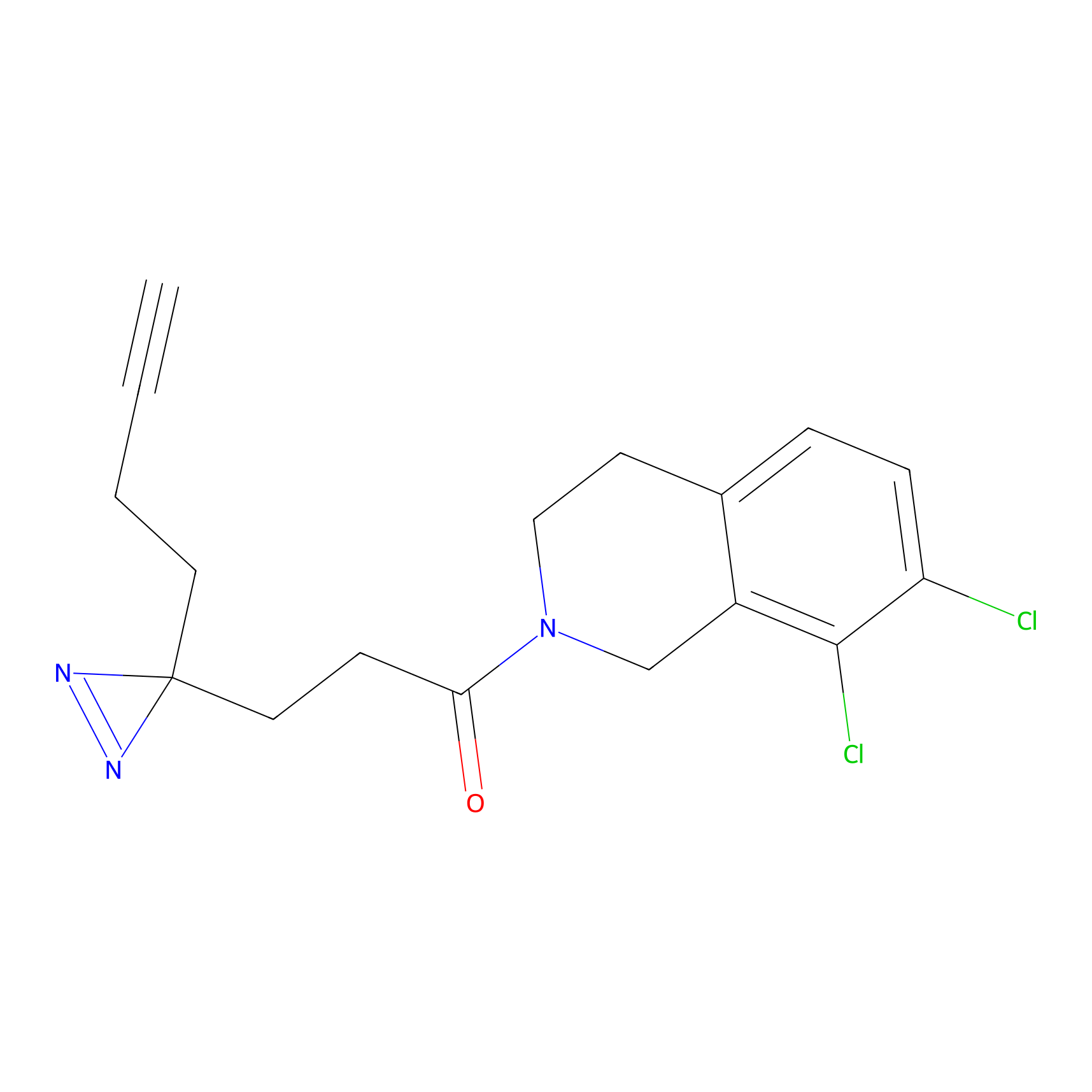
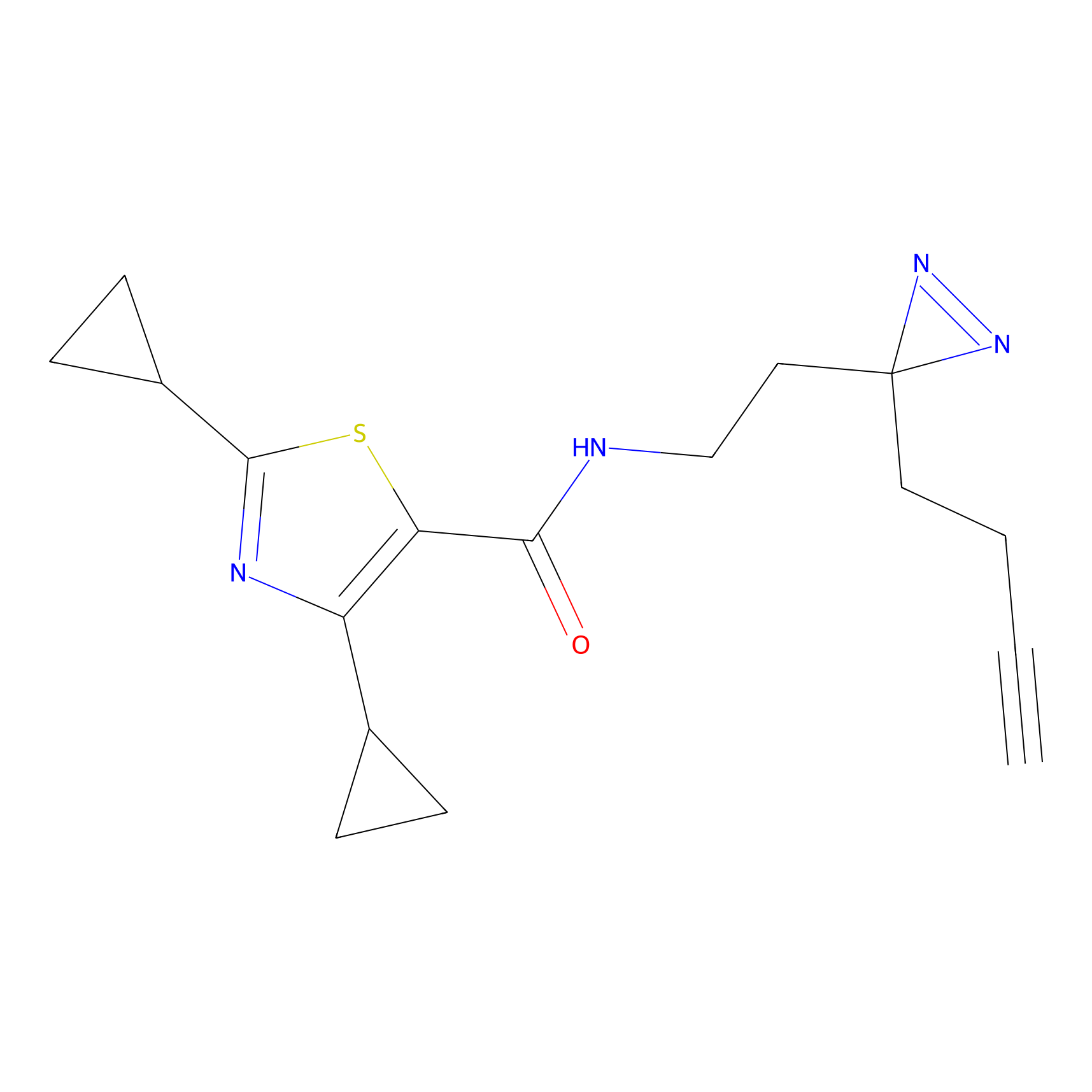
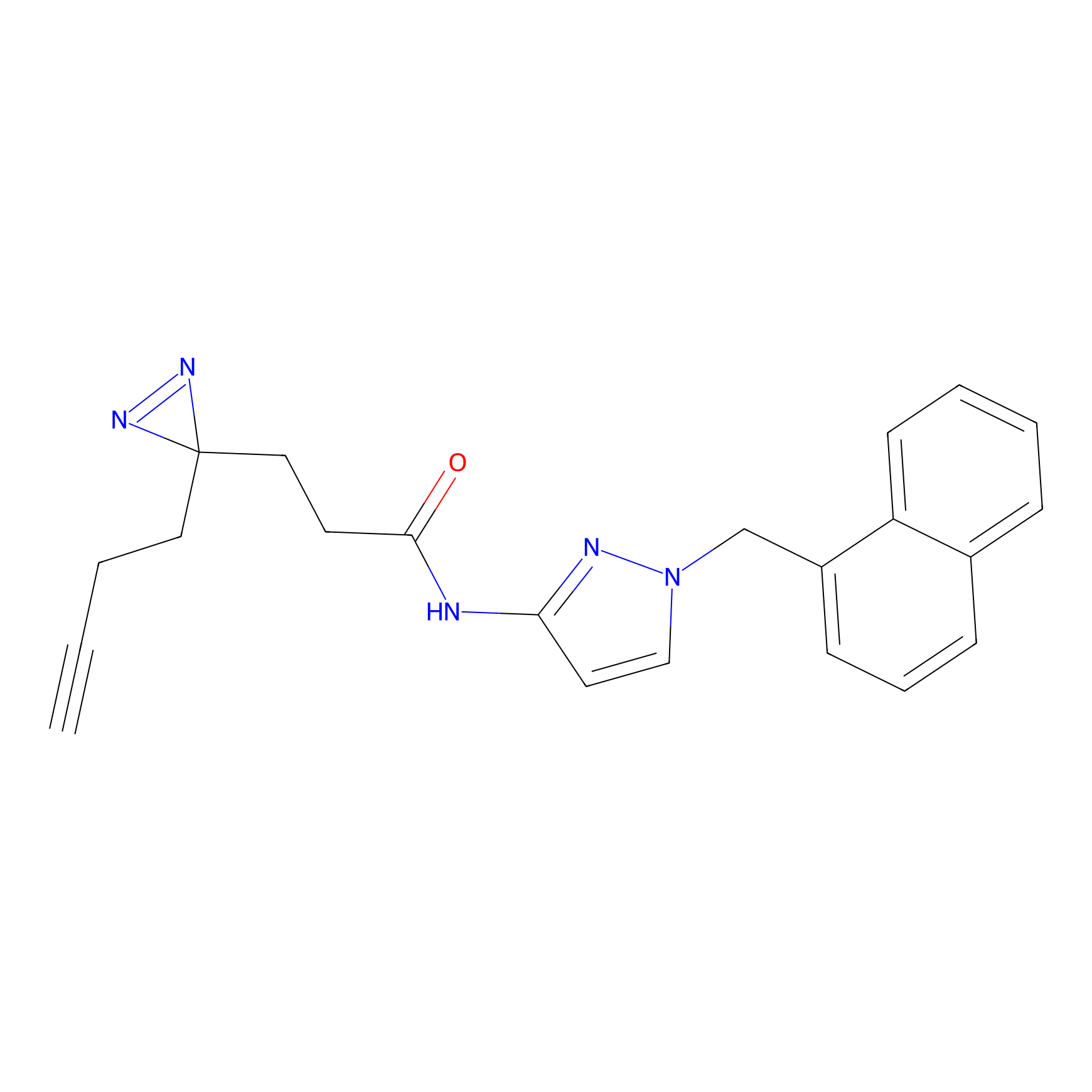
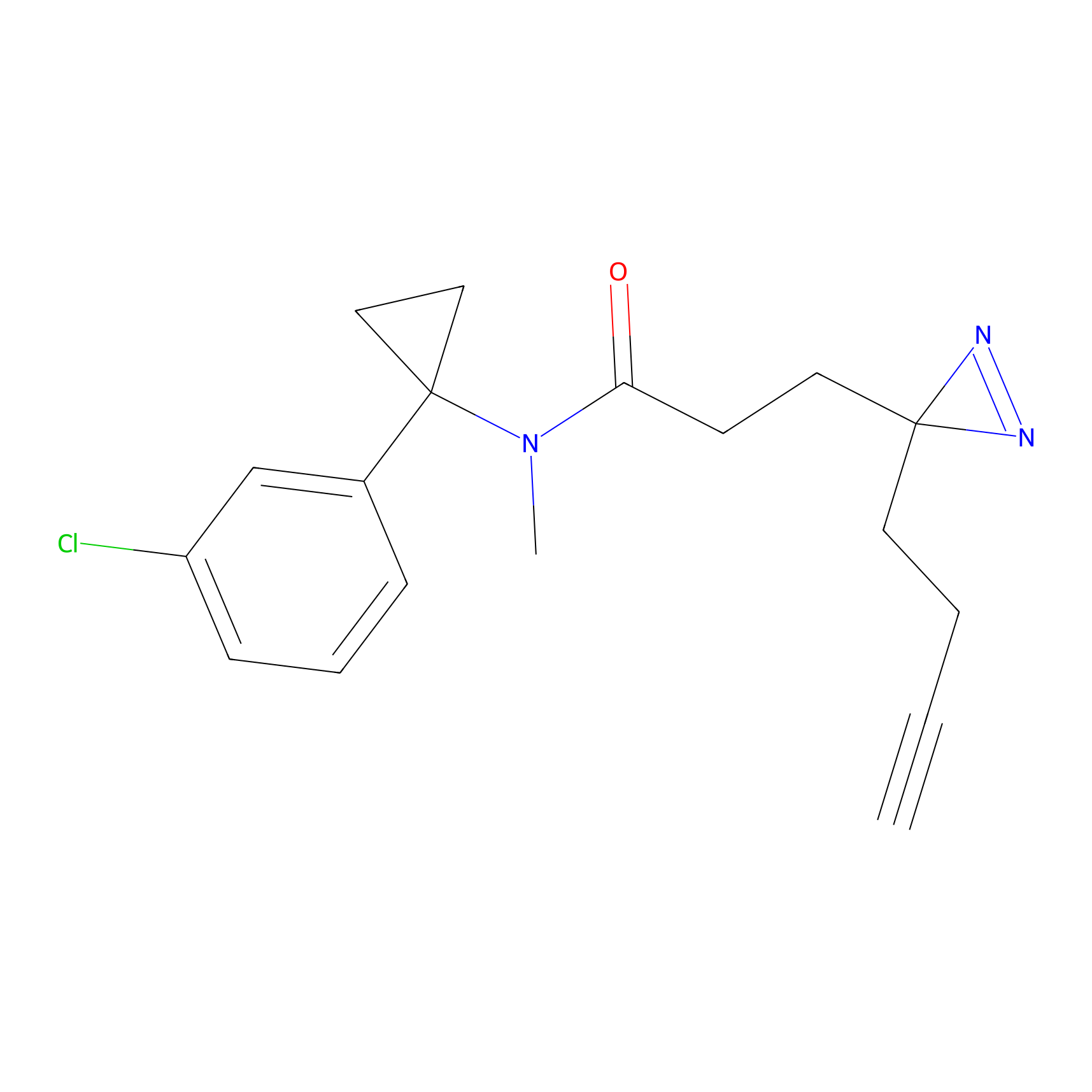
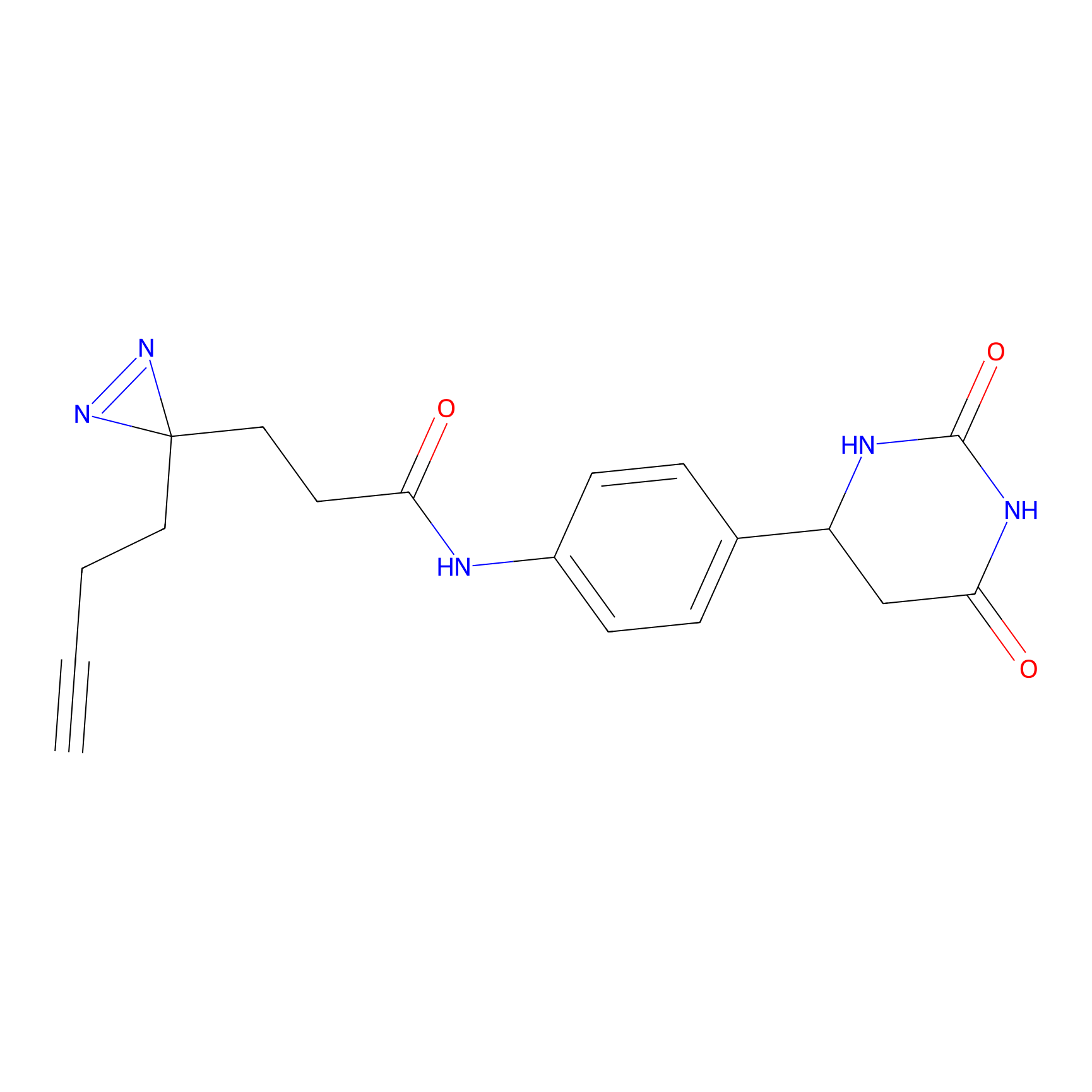
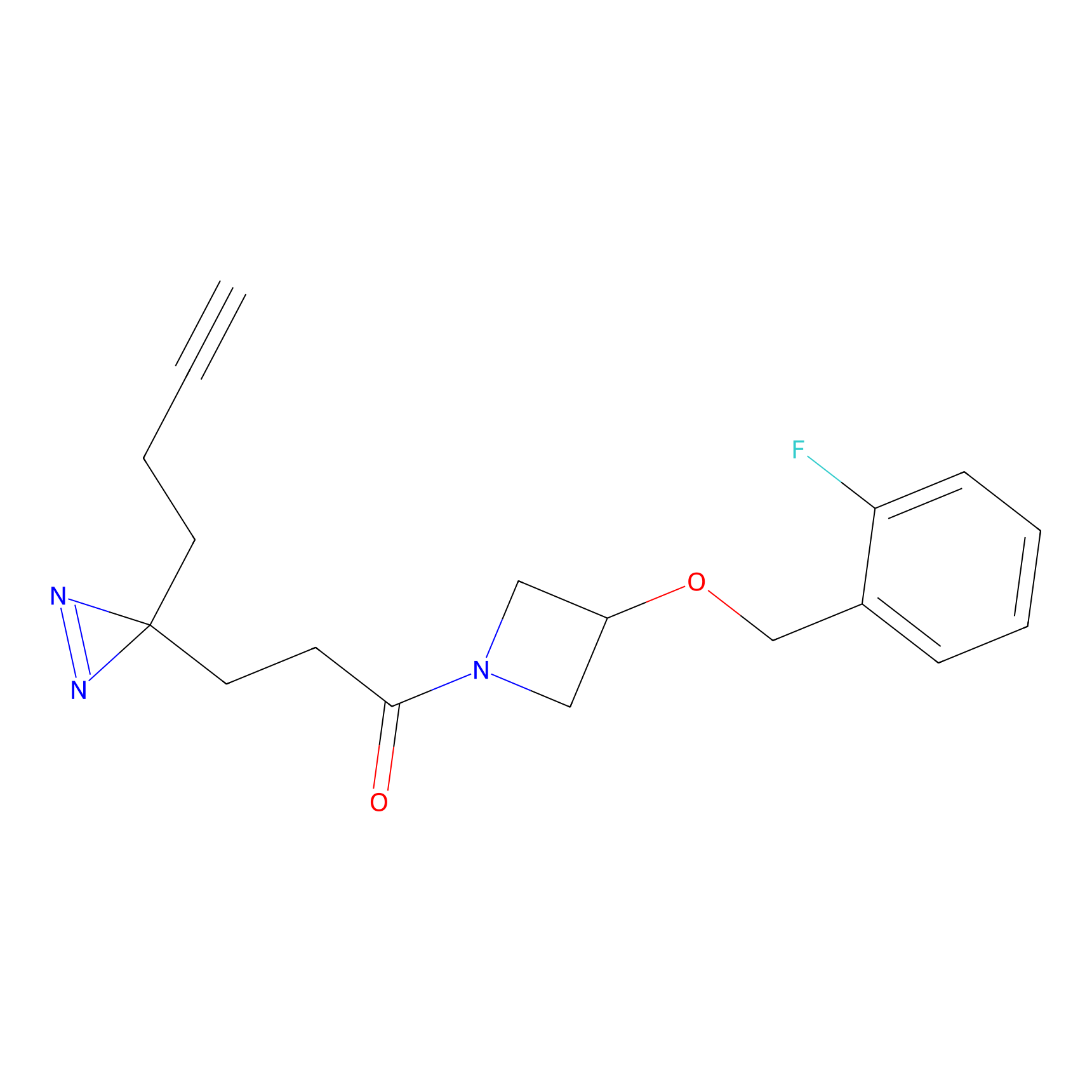
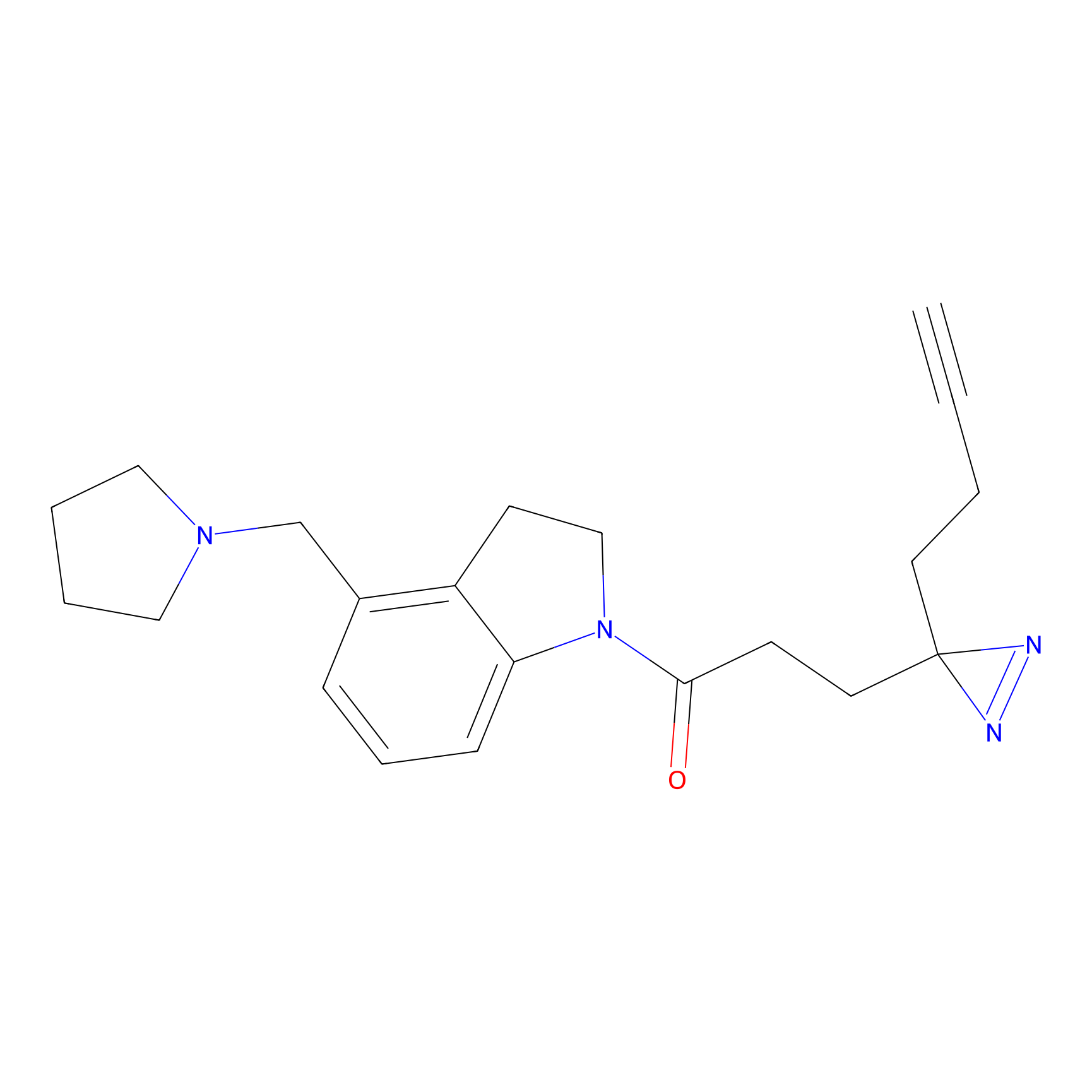
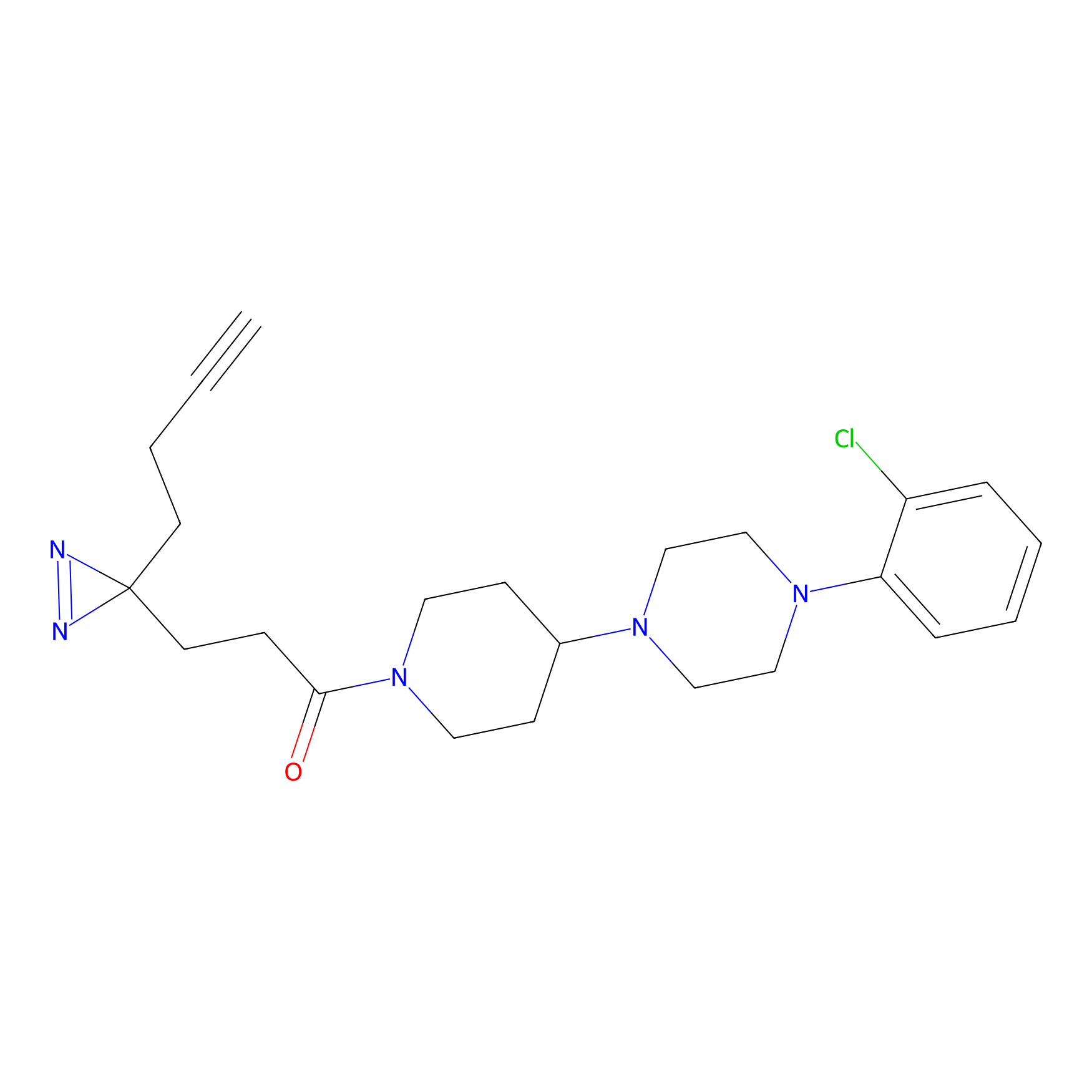
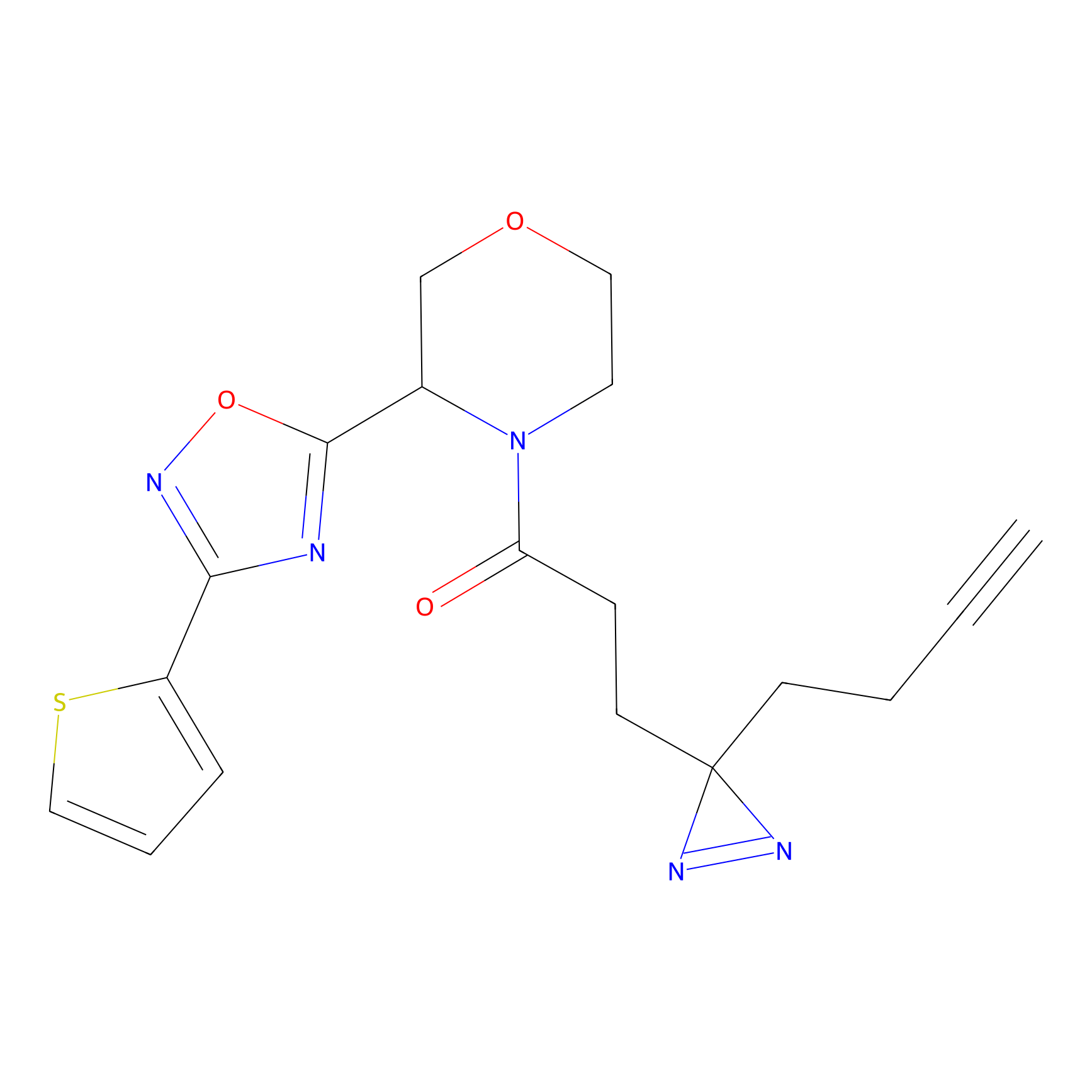
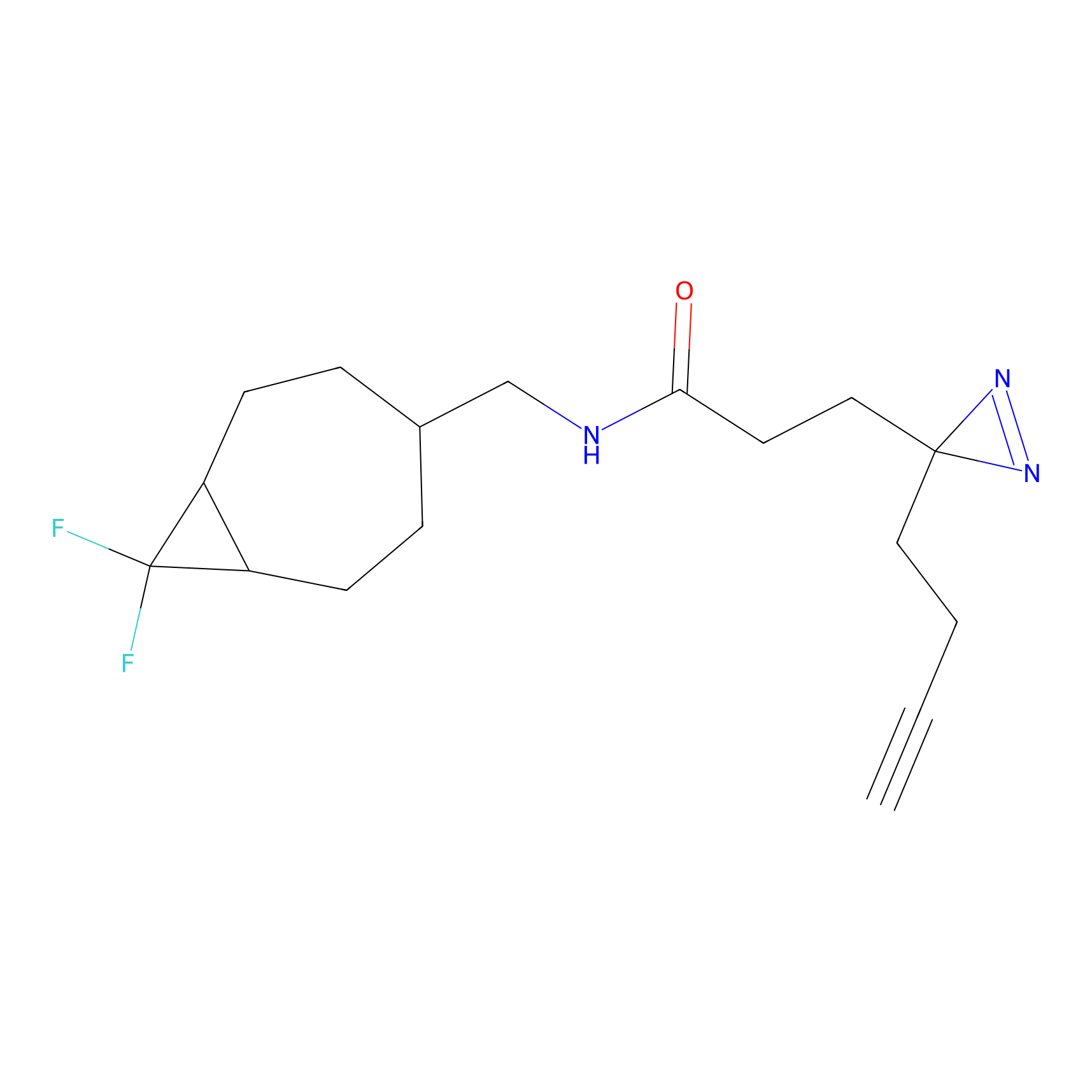
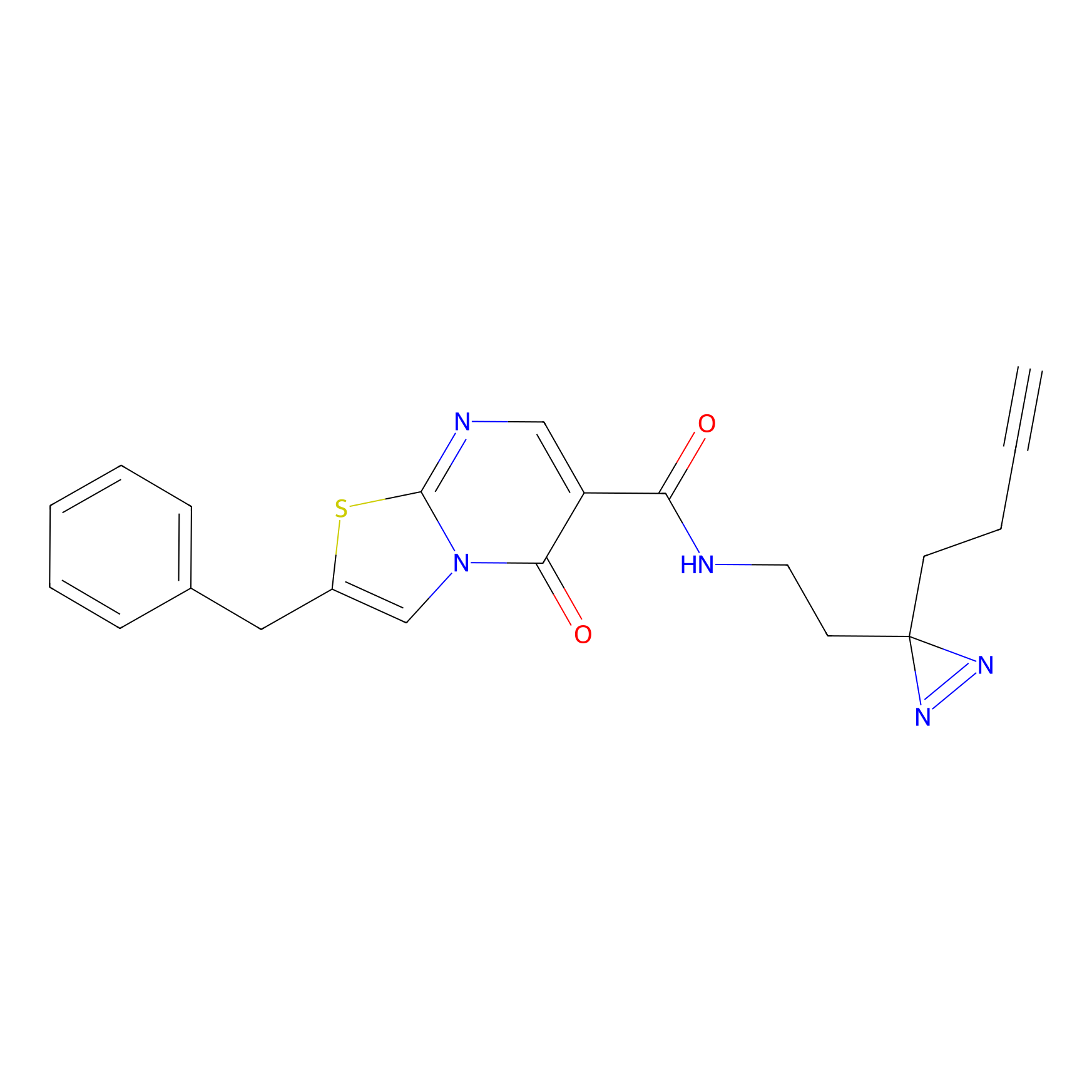
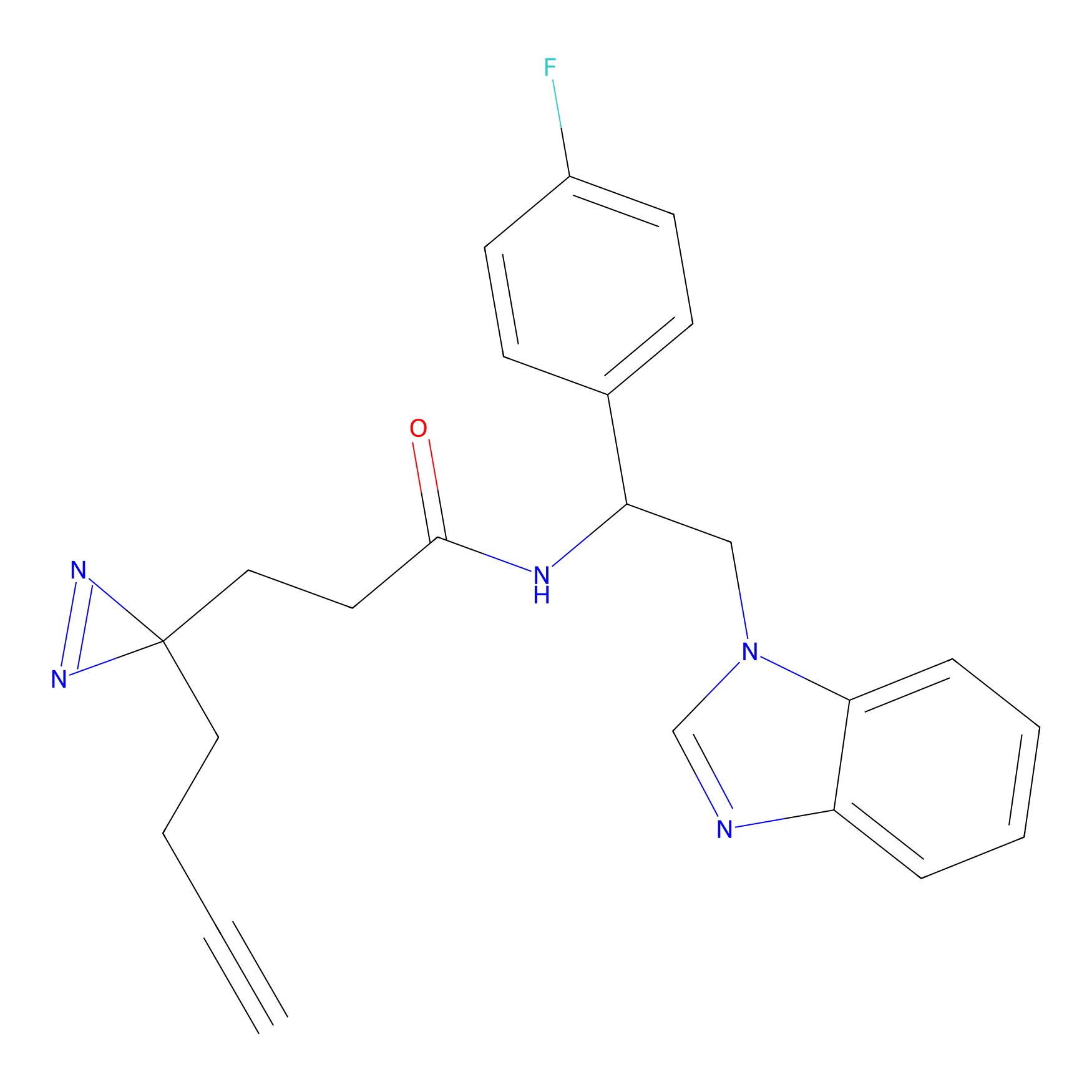
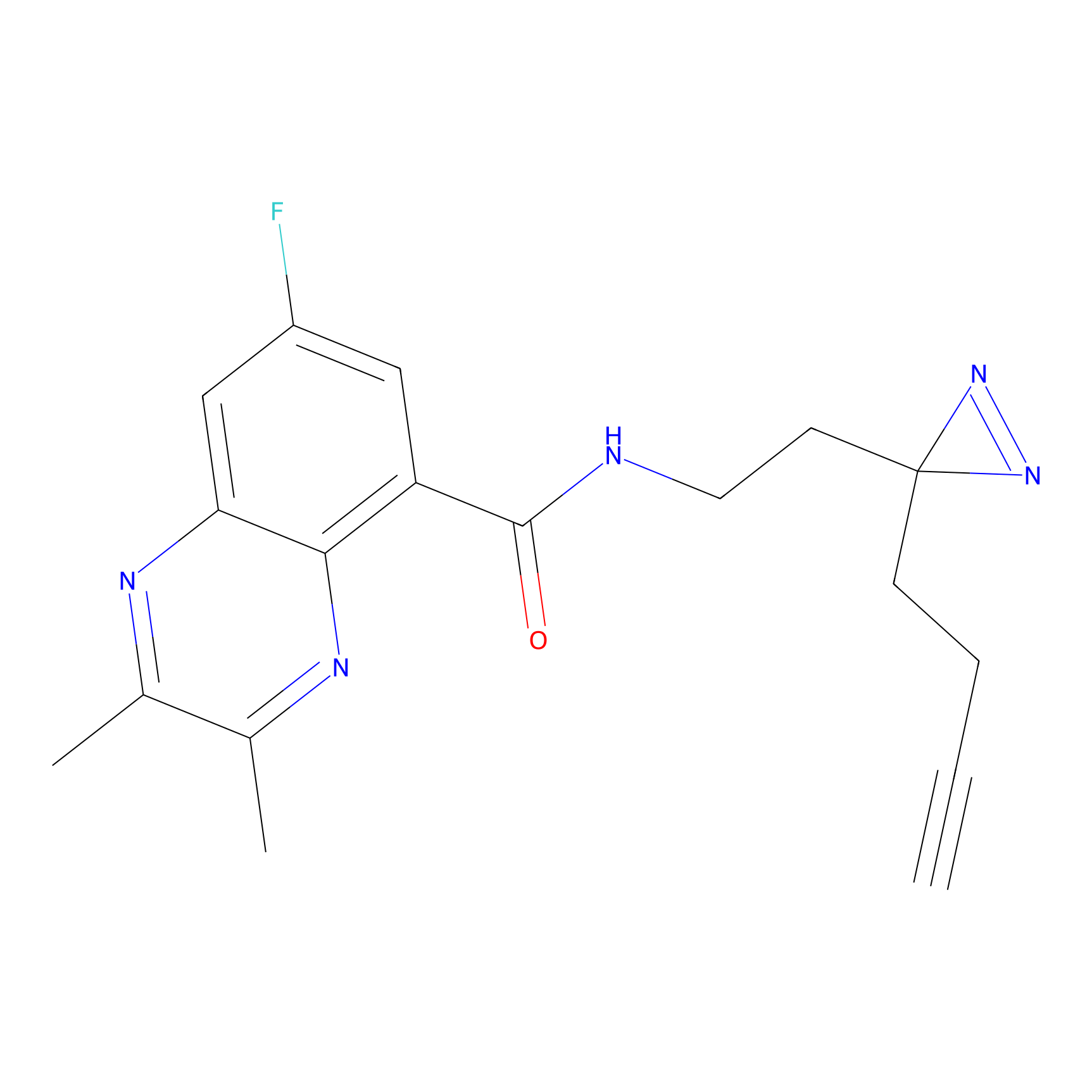
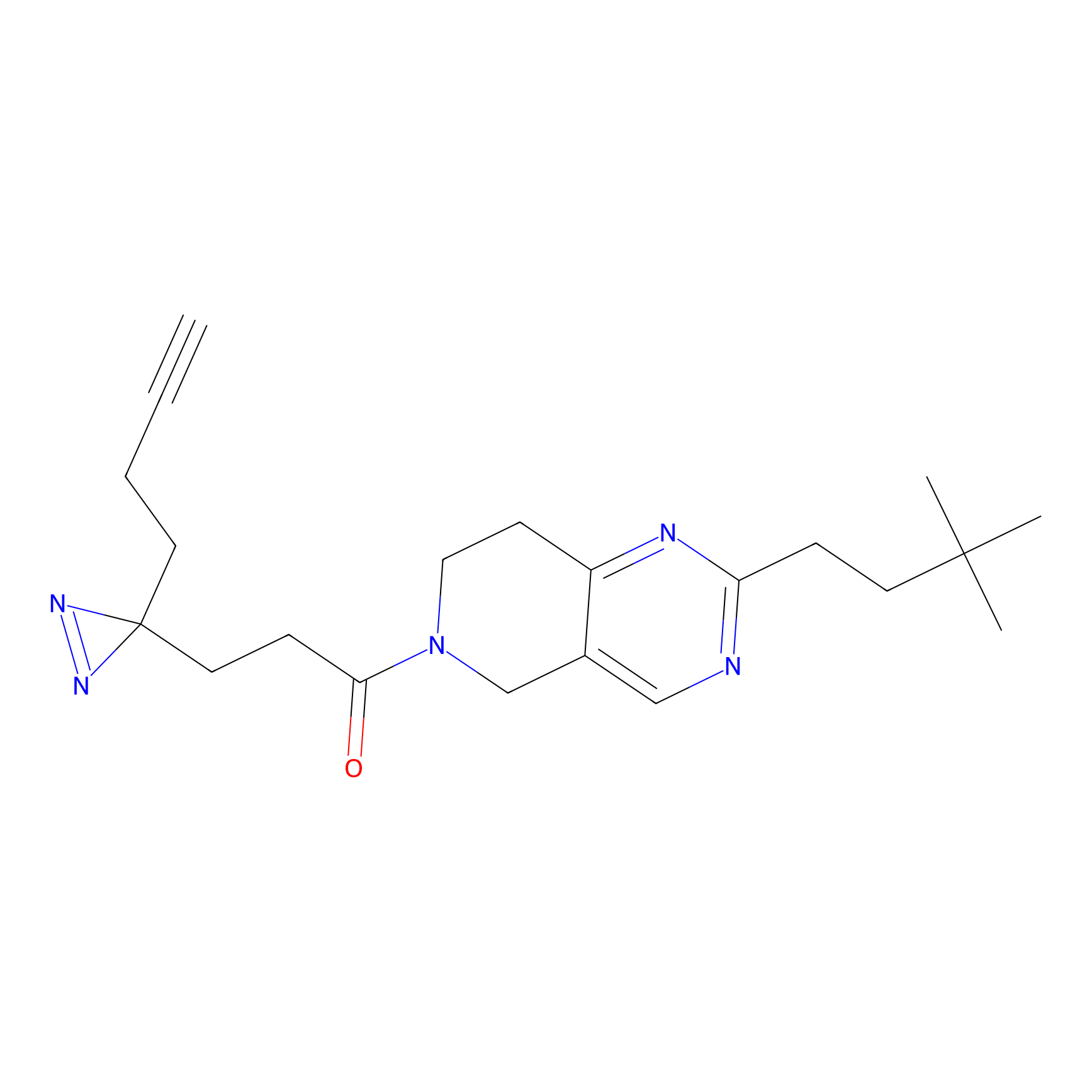
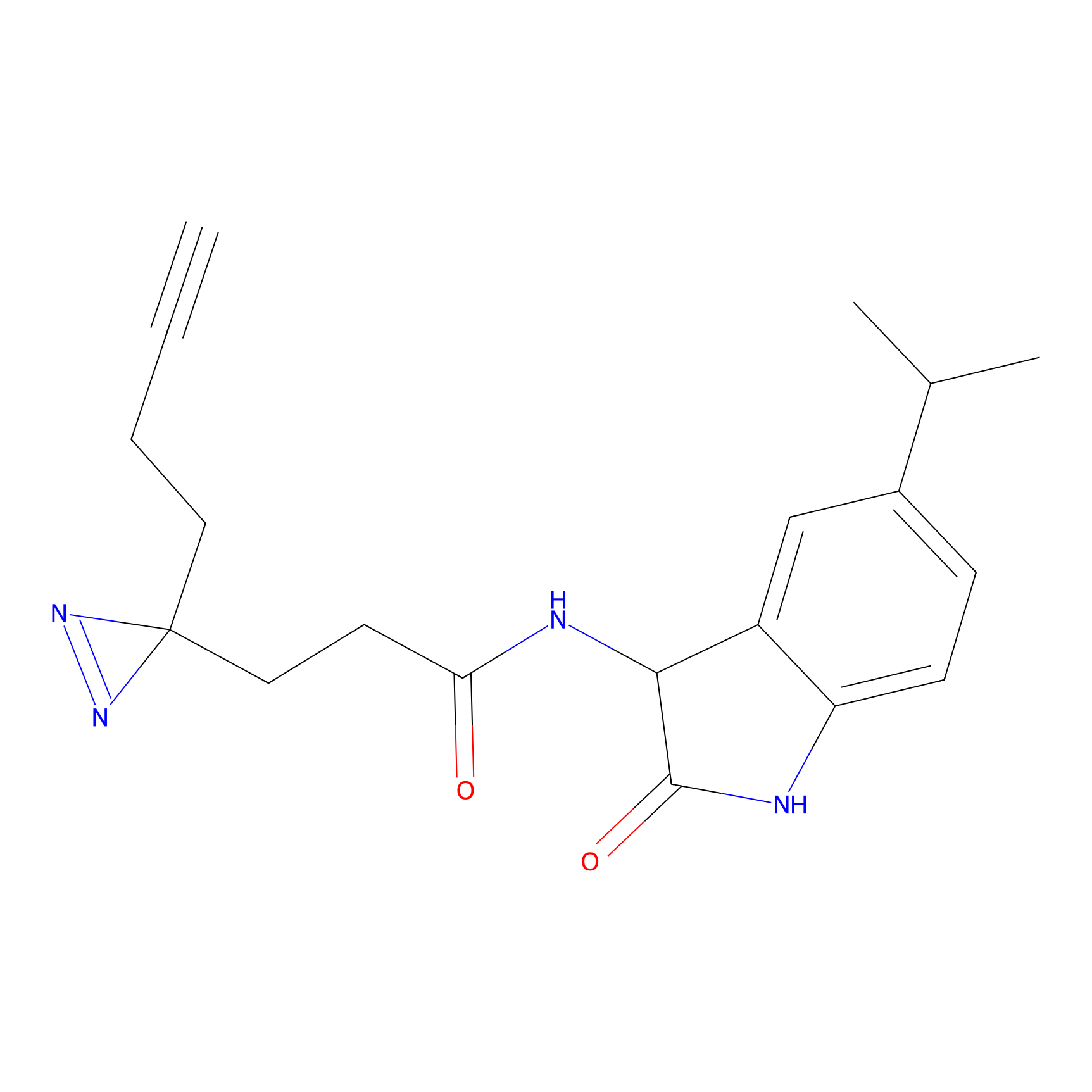
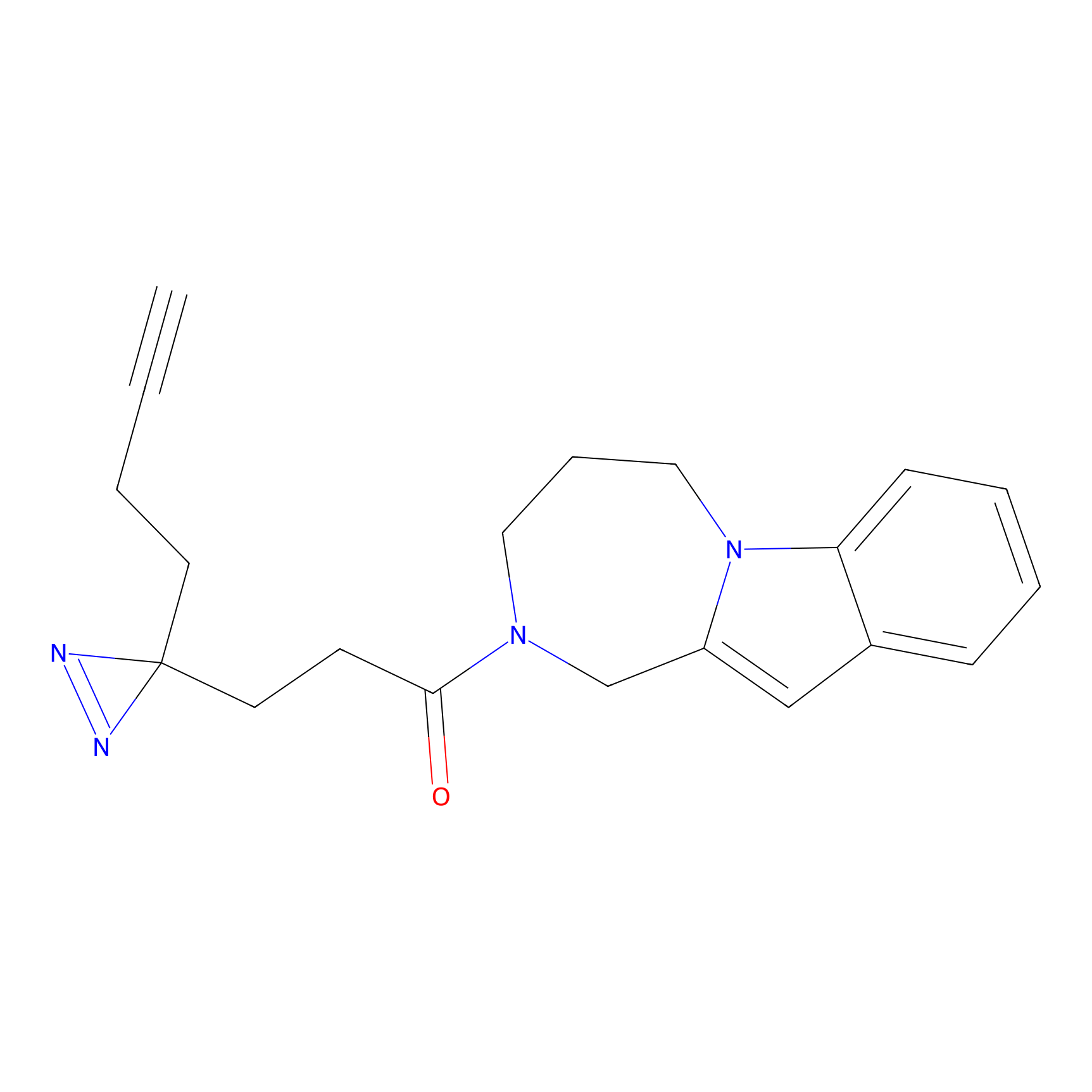
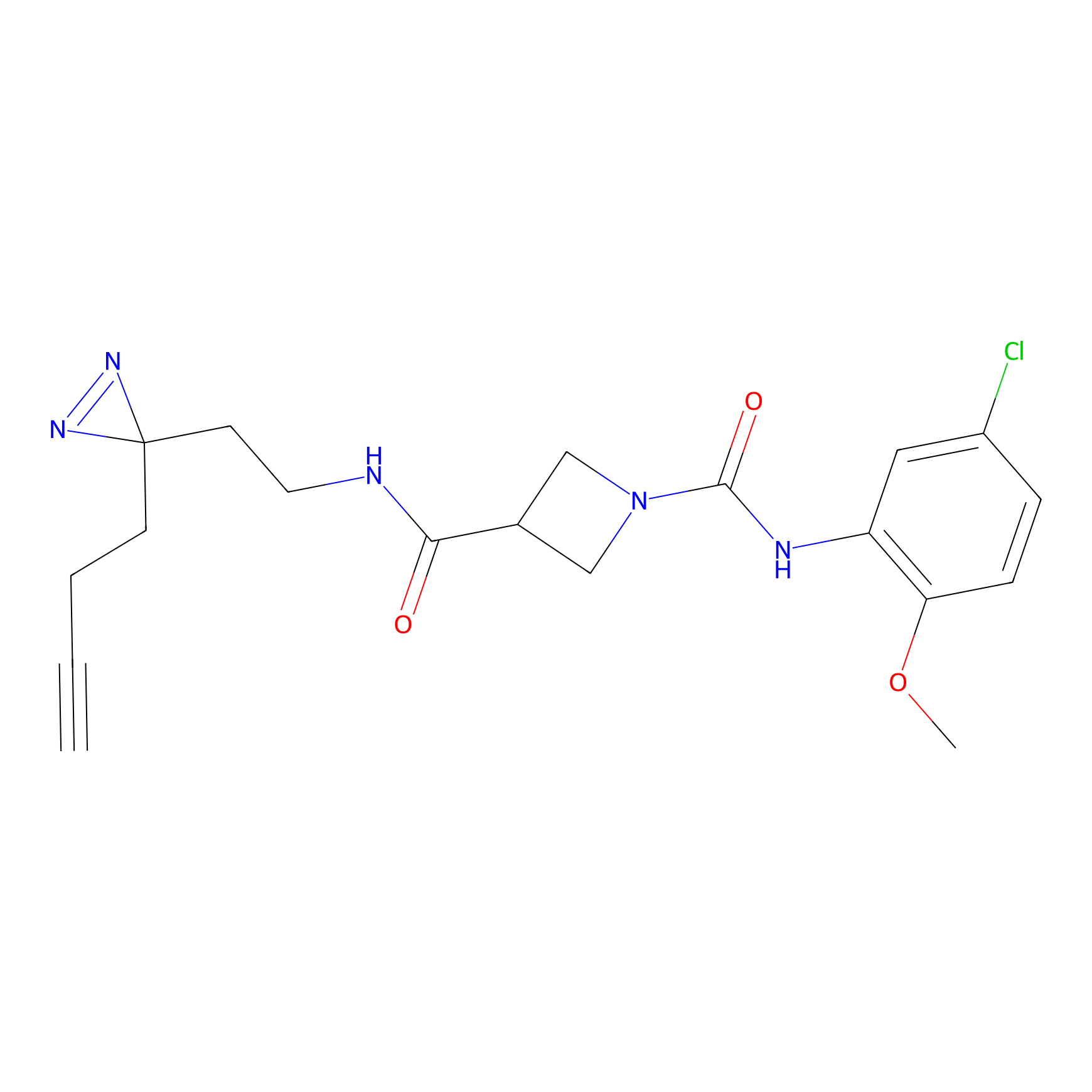
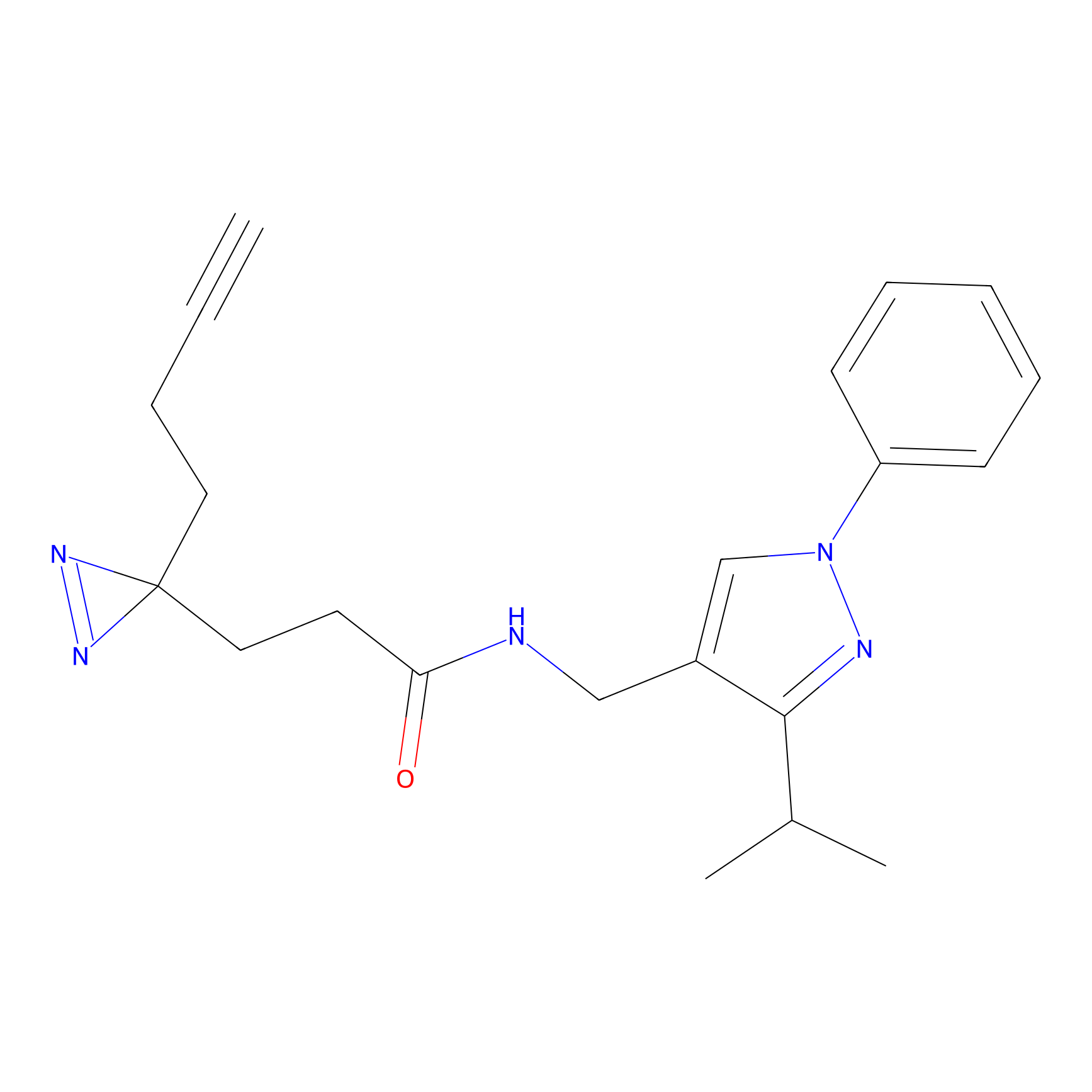
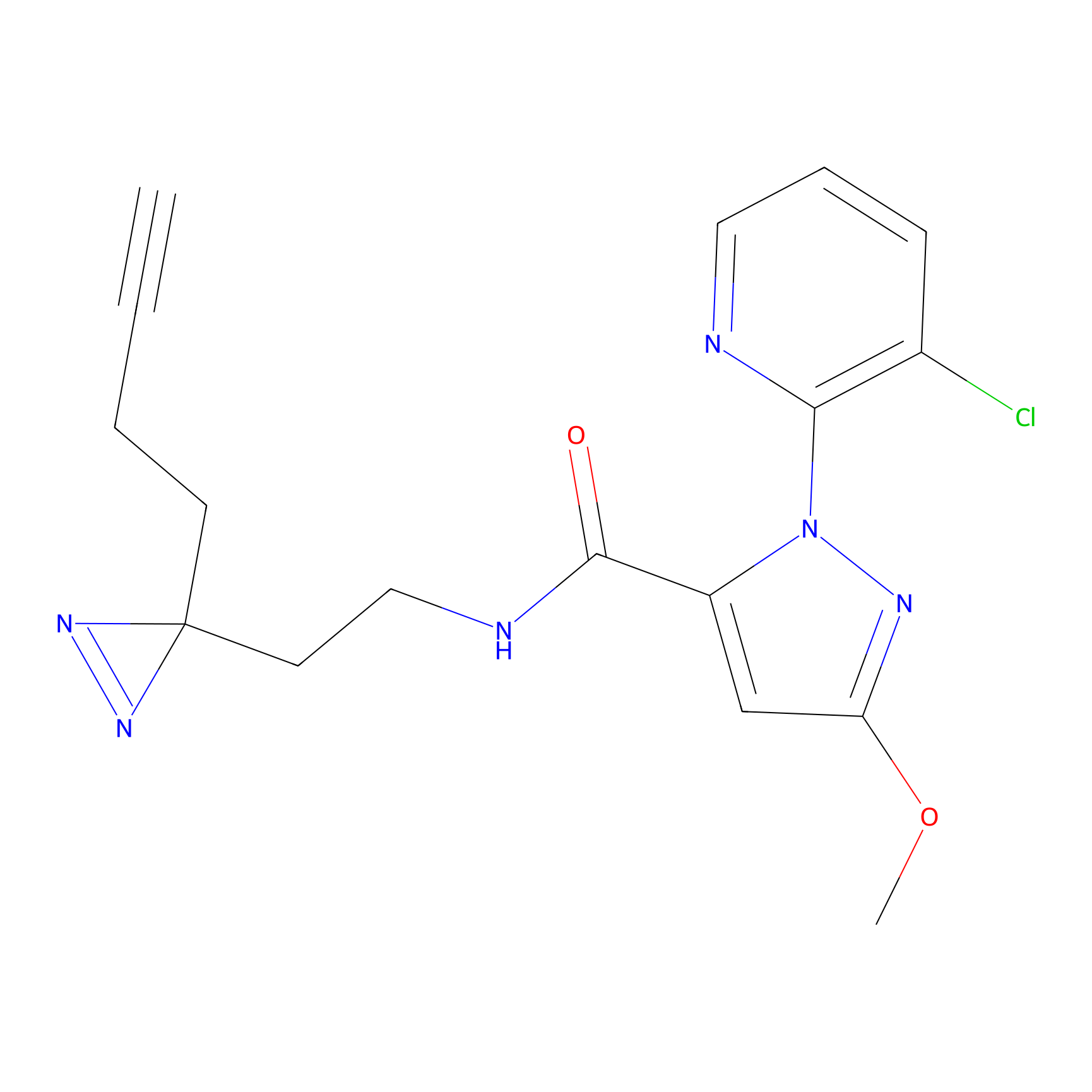
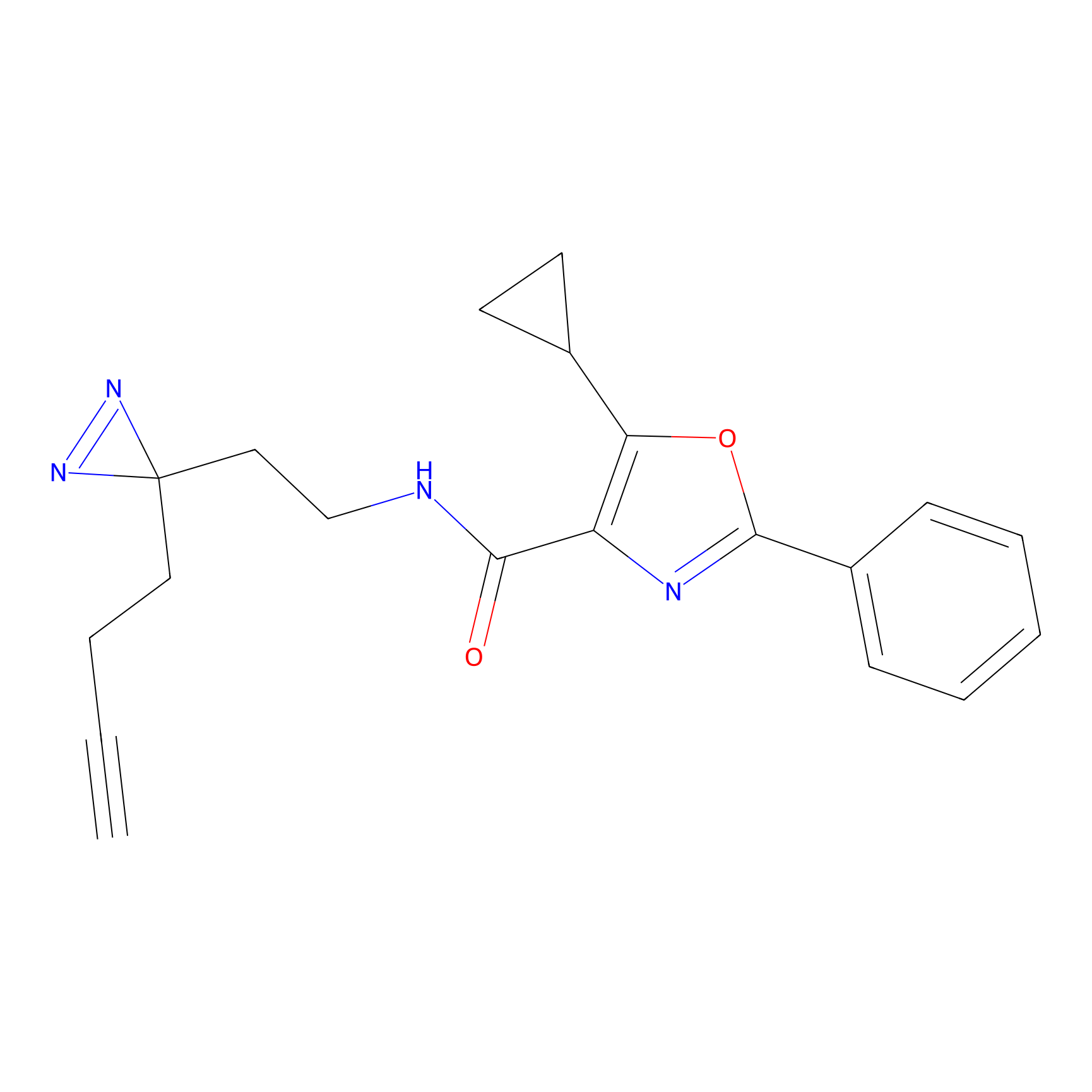
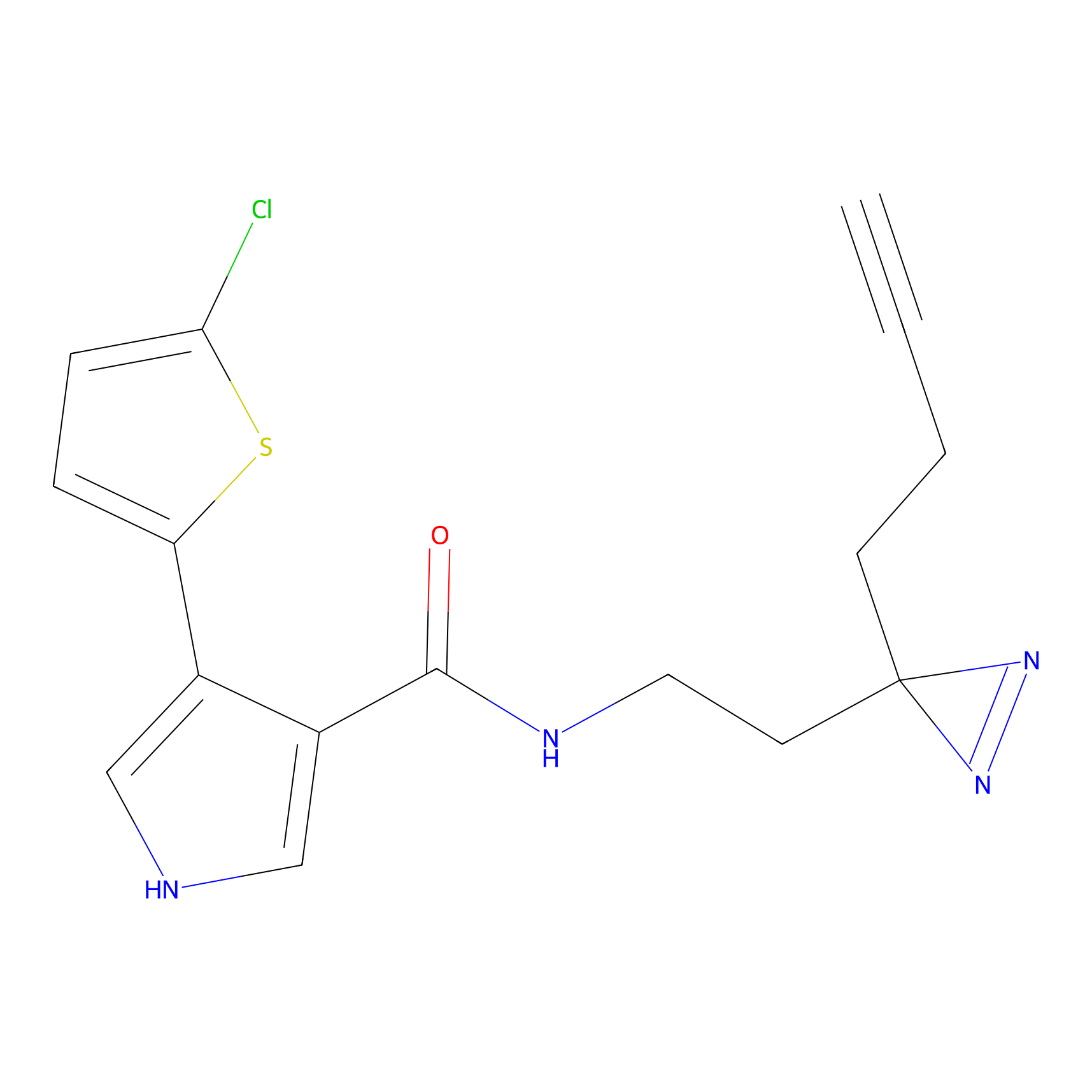
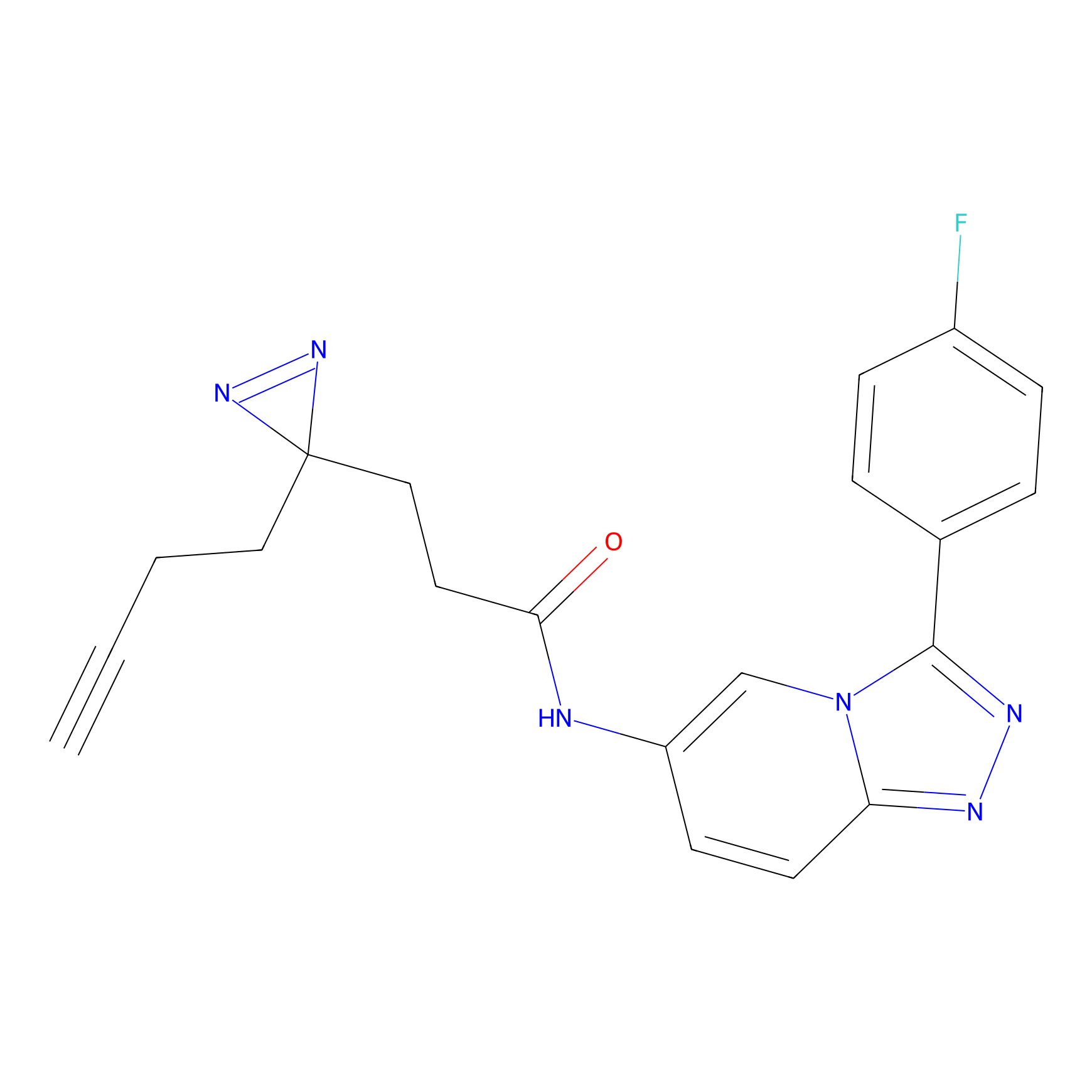
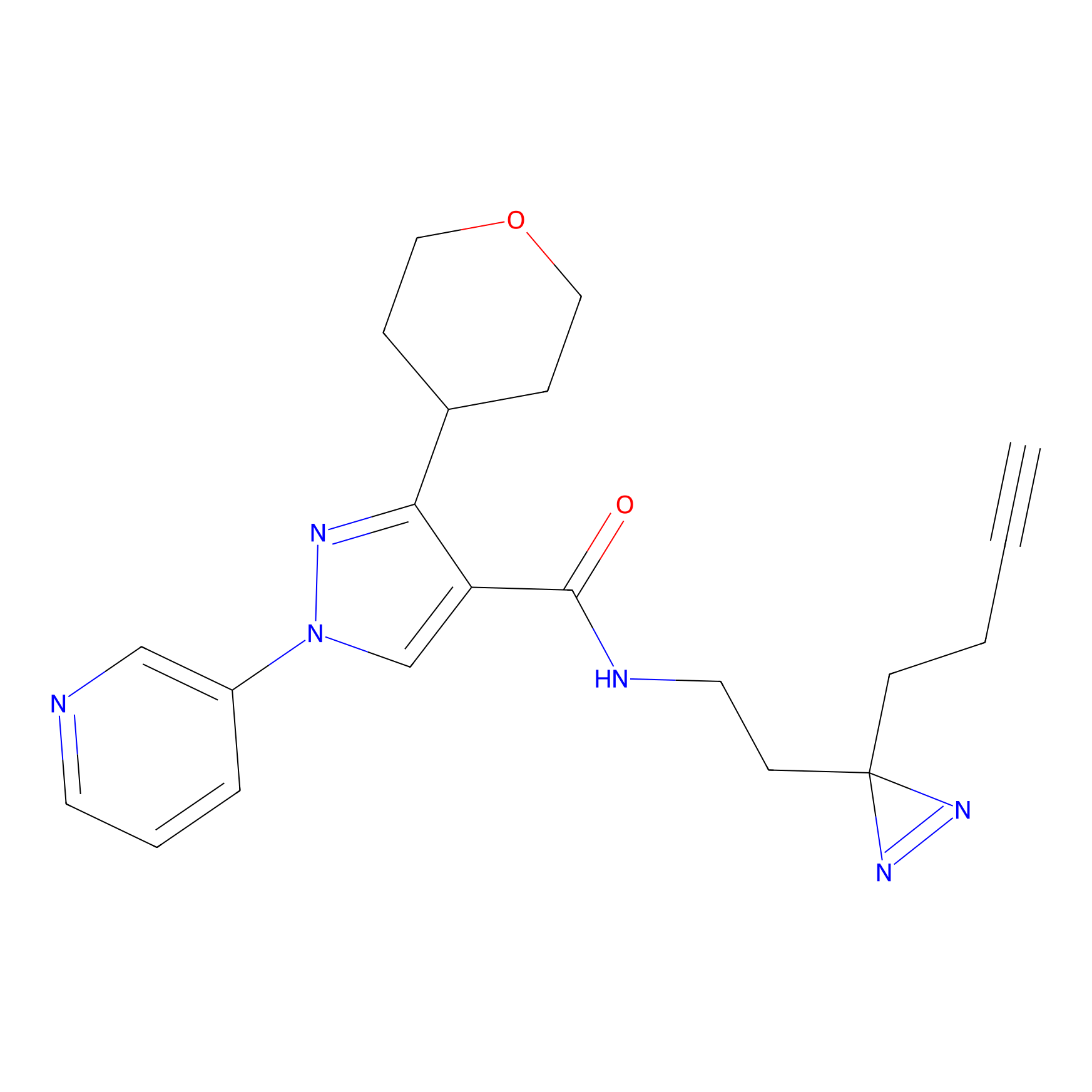
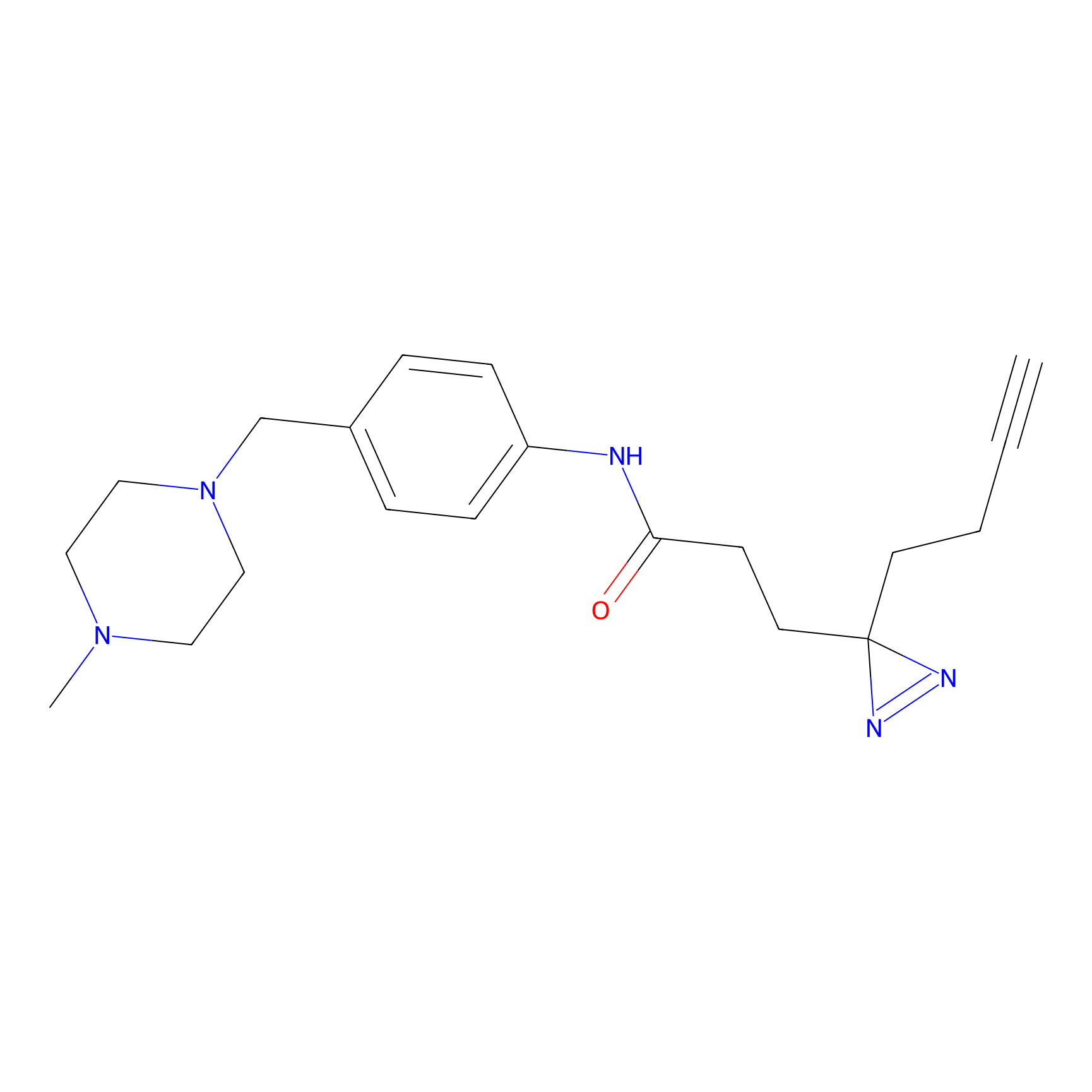
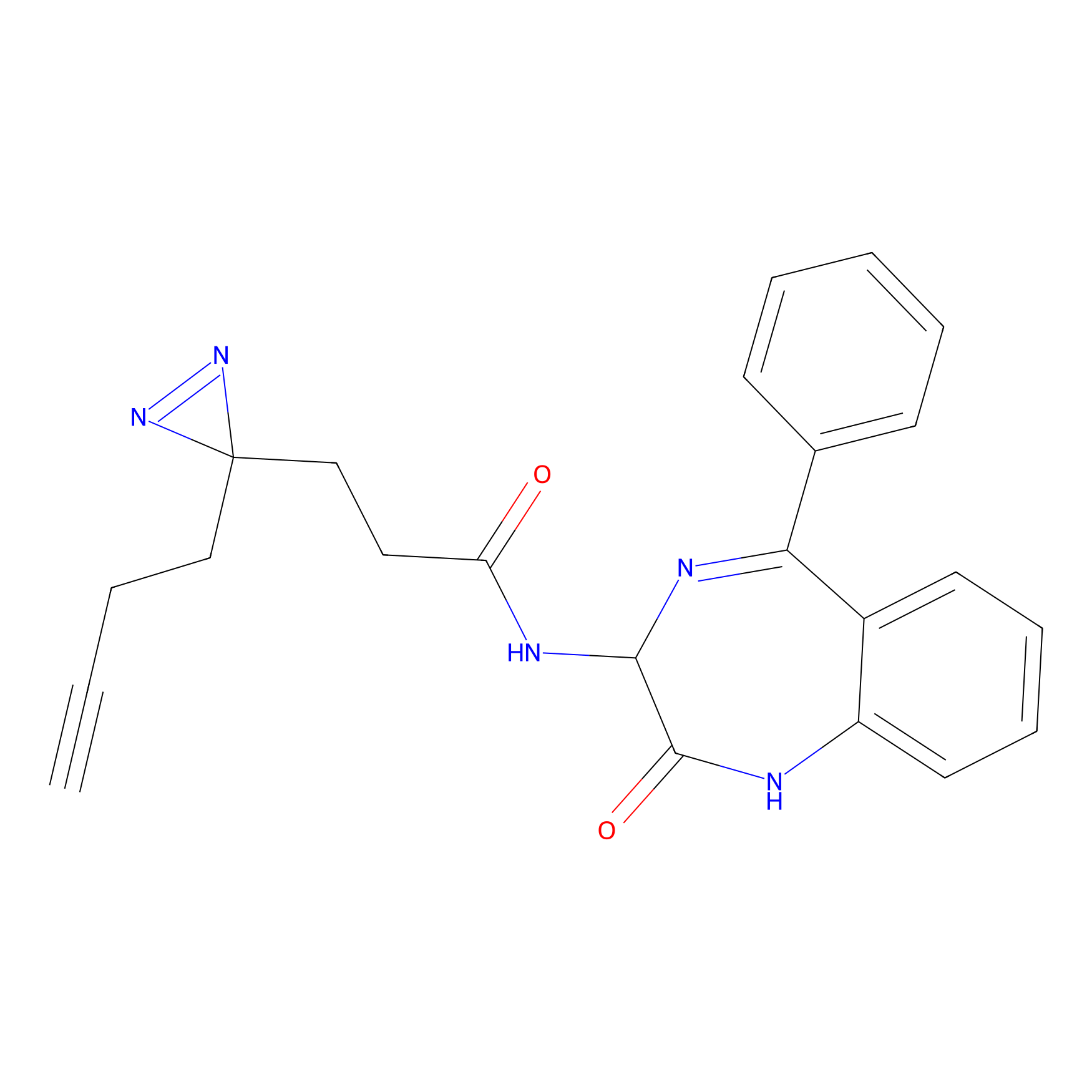
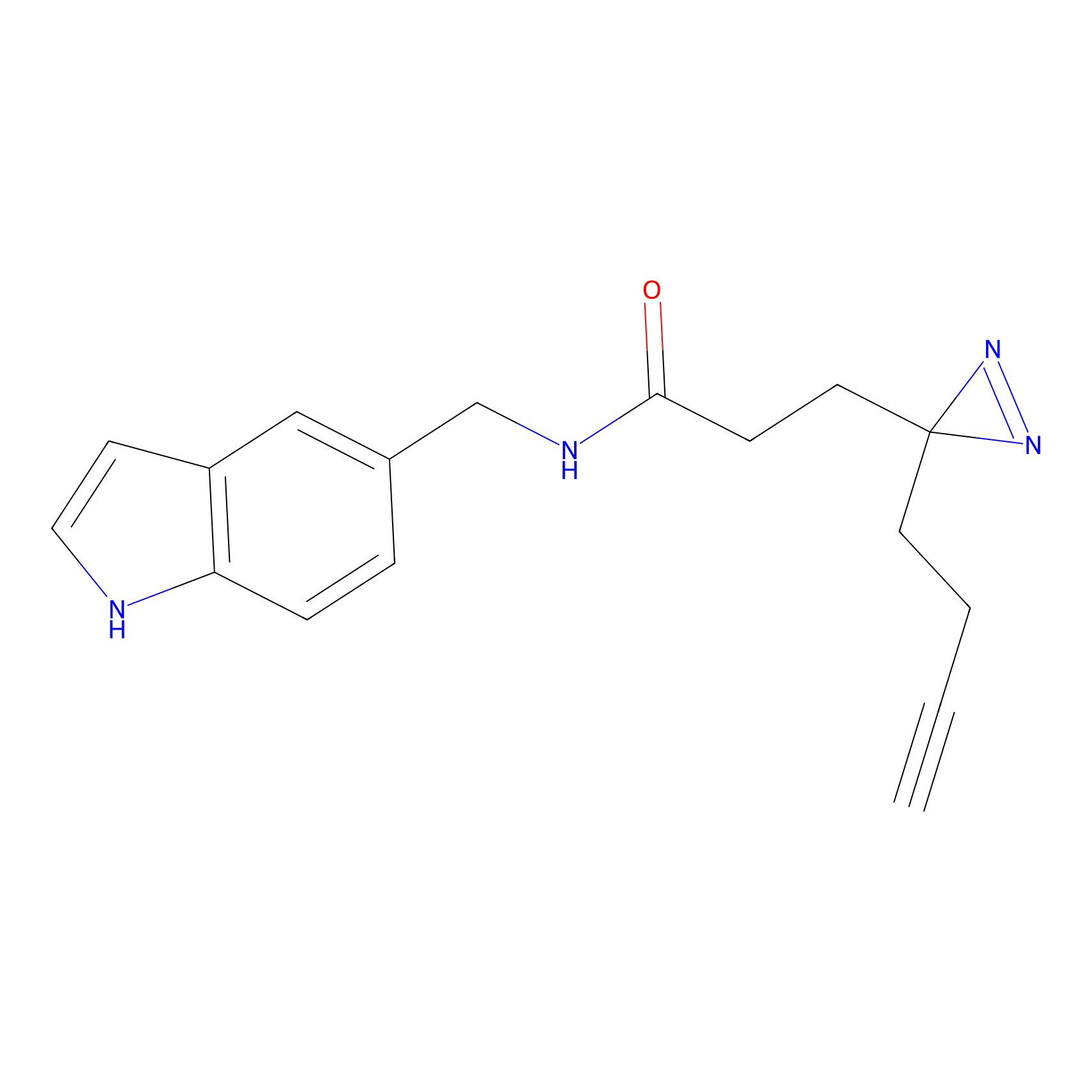
FBPP2 Probe Info |
 |
21.44 | LDD0318 | [1] | |
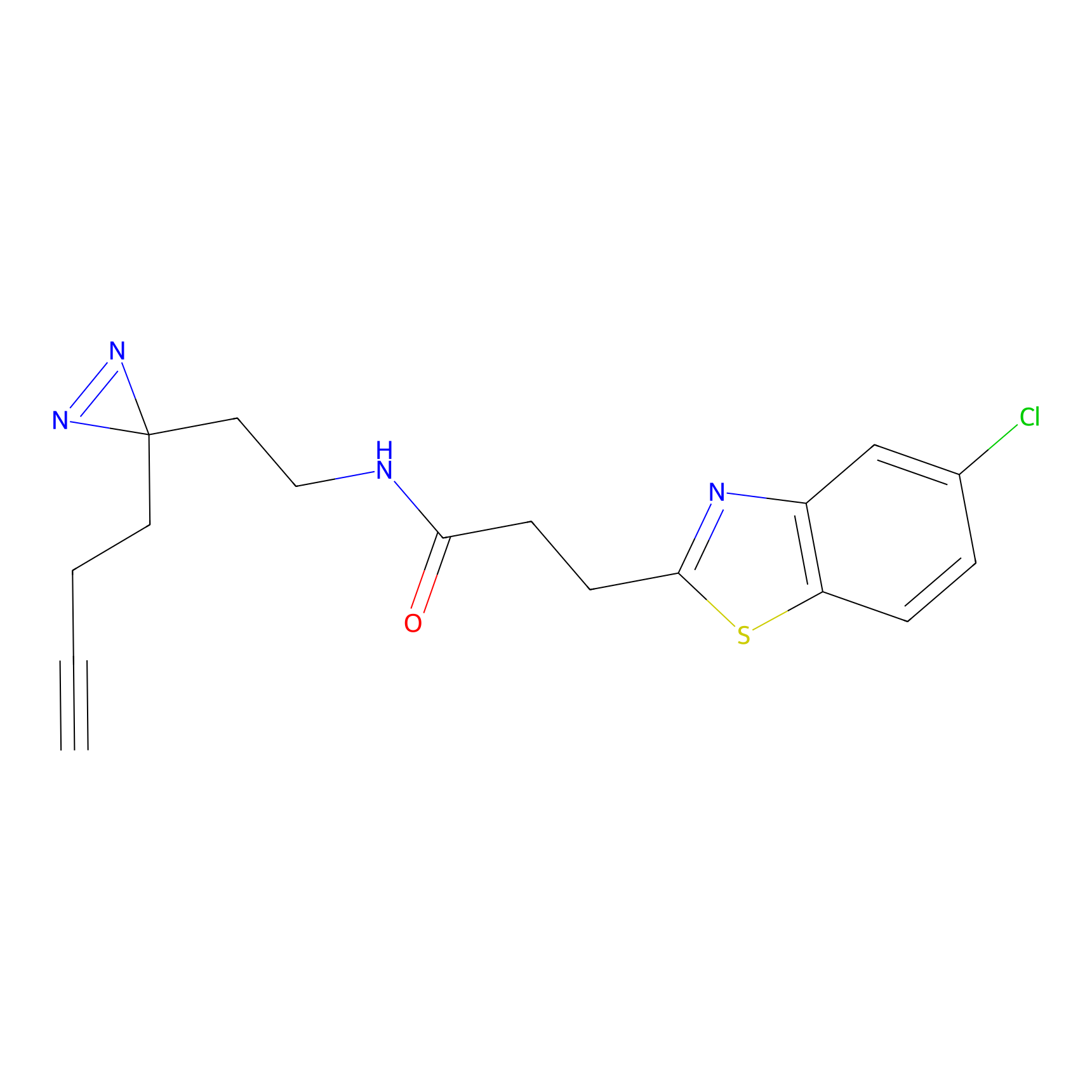
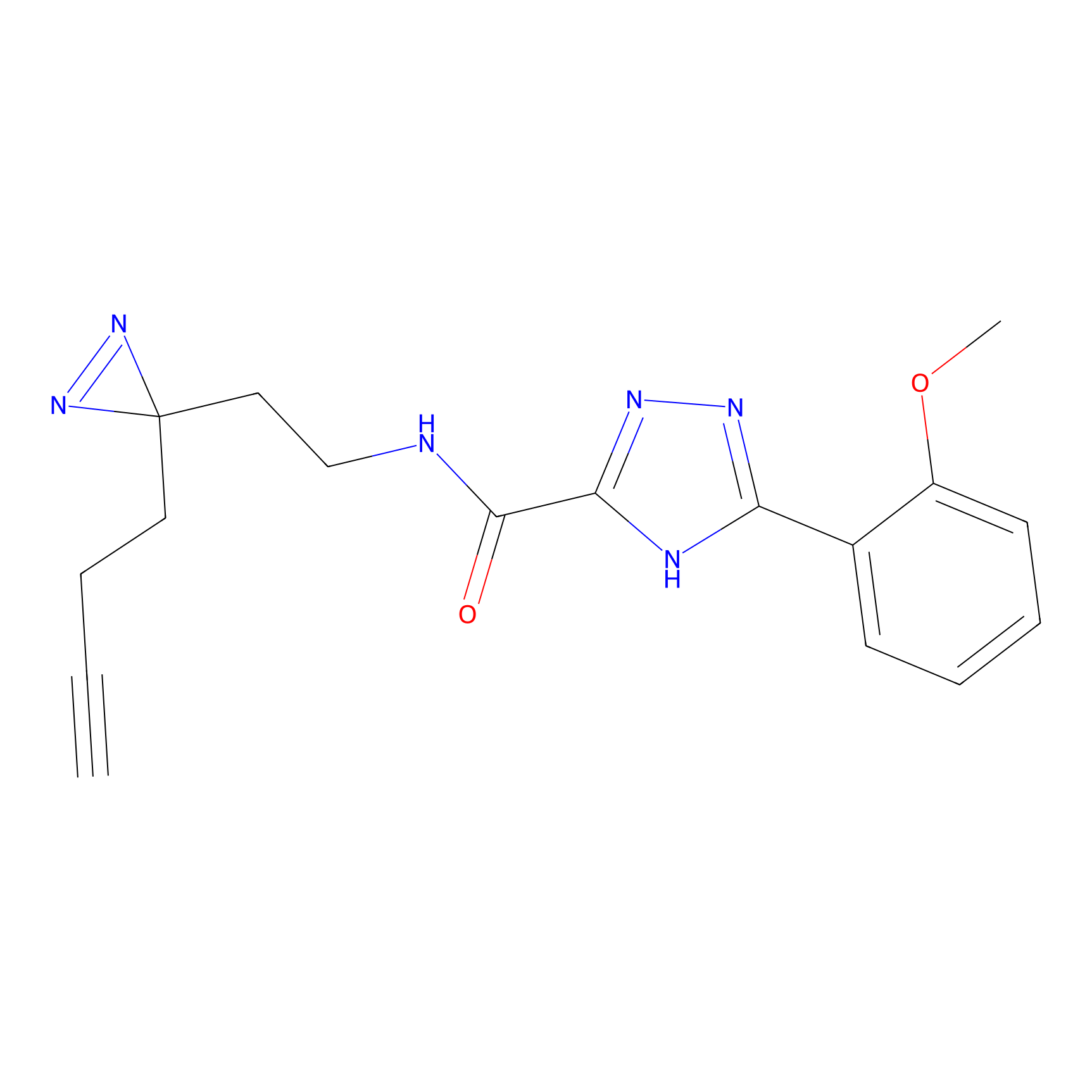
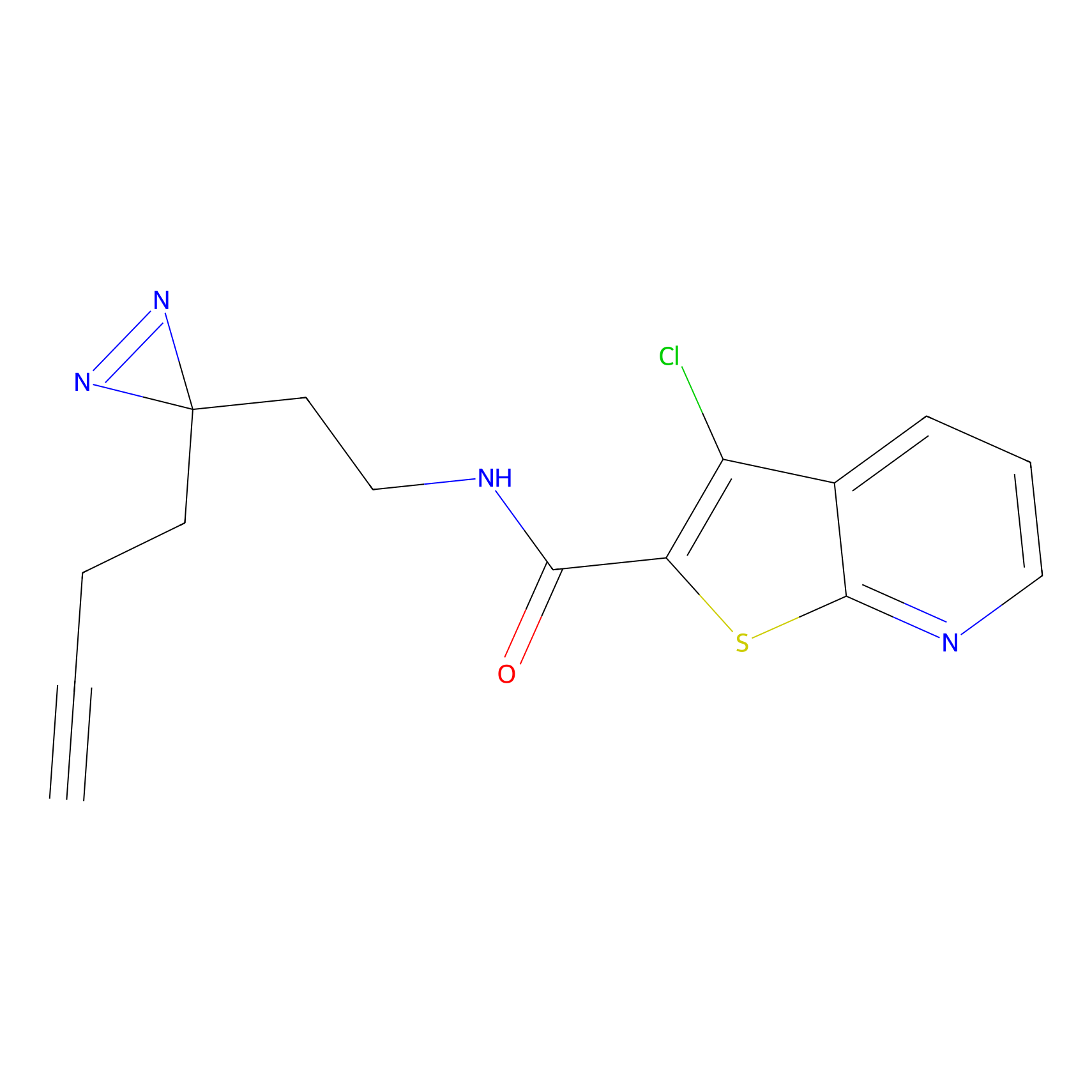
|
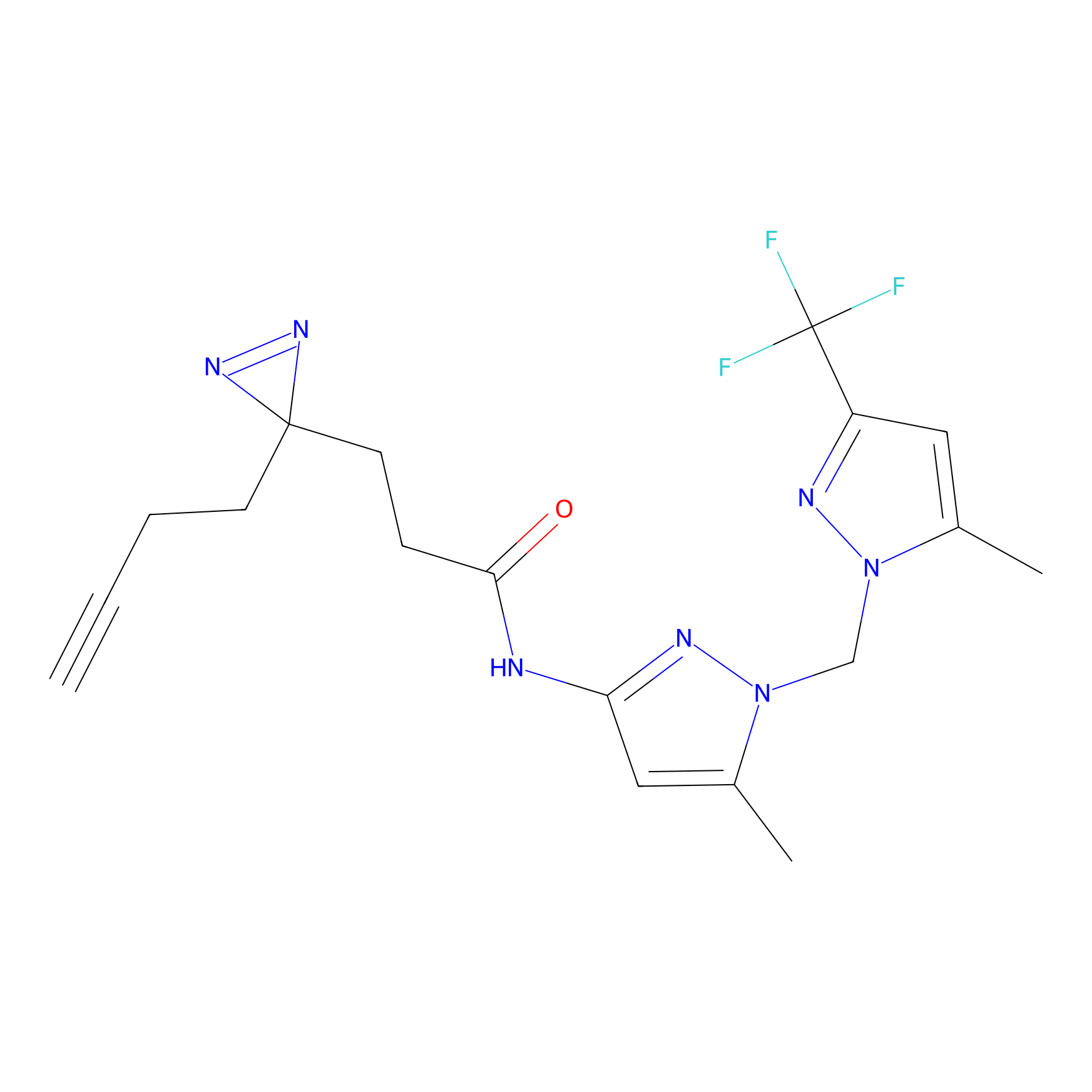
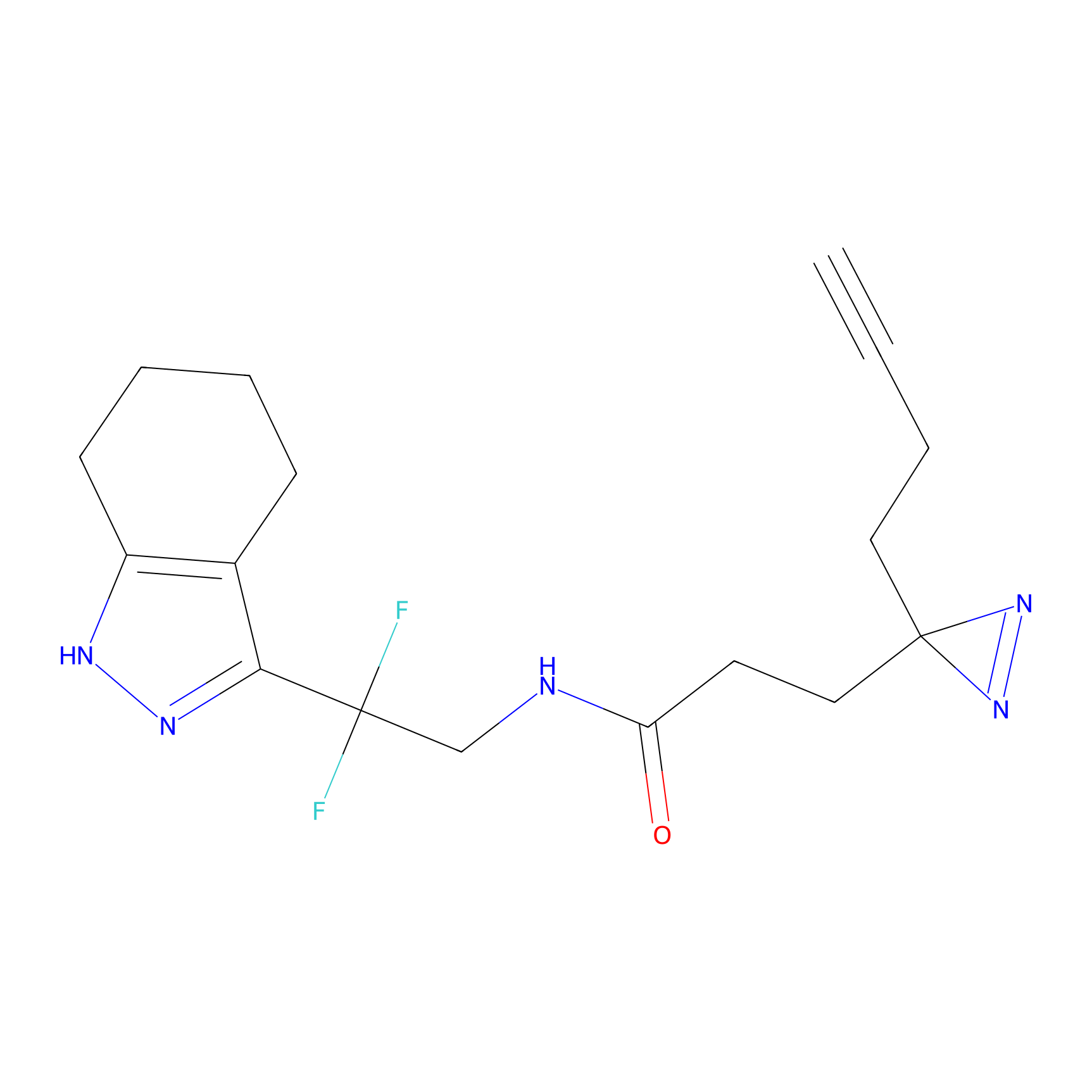
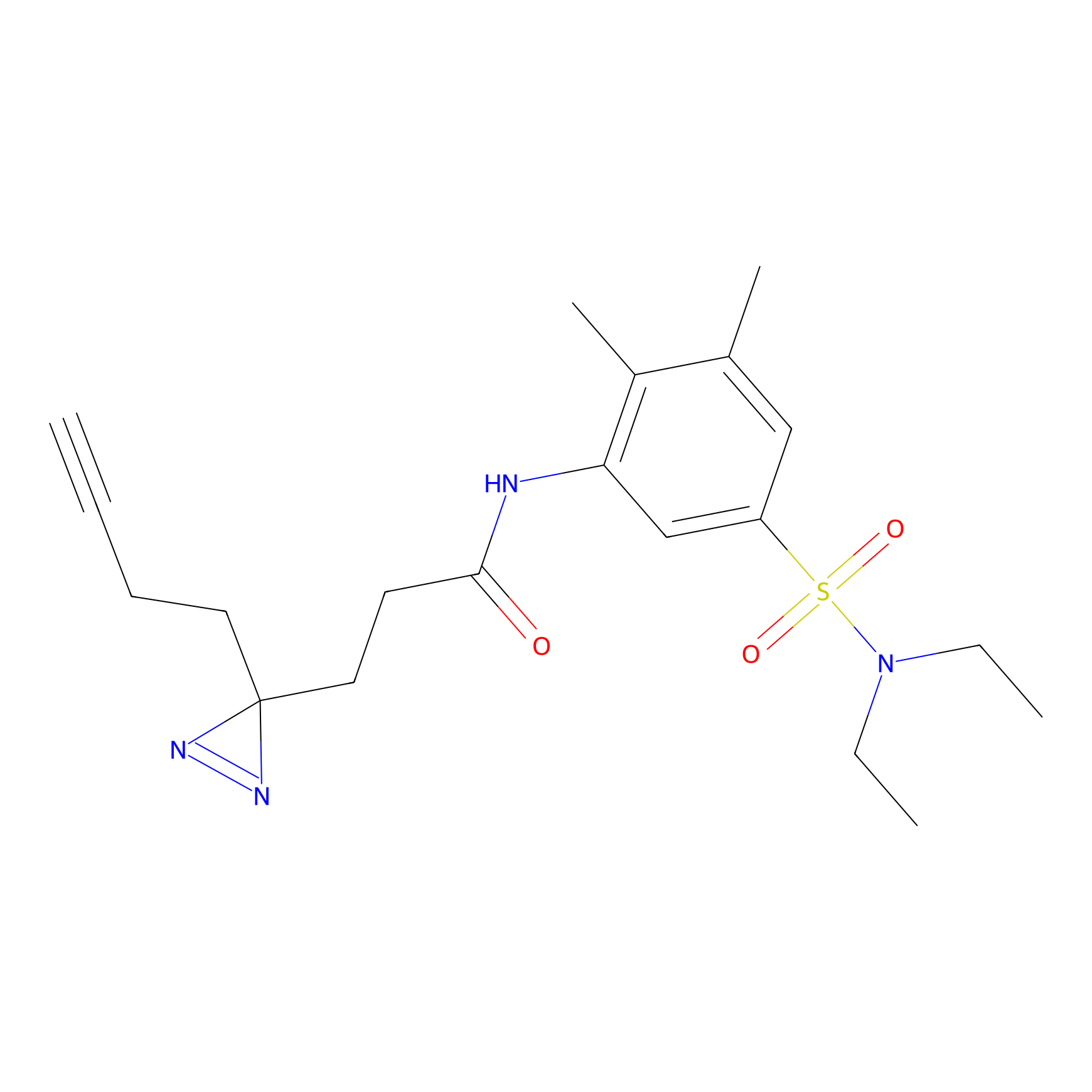
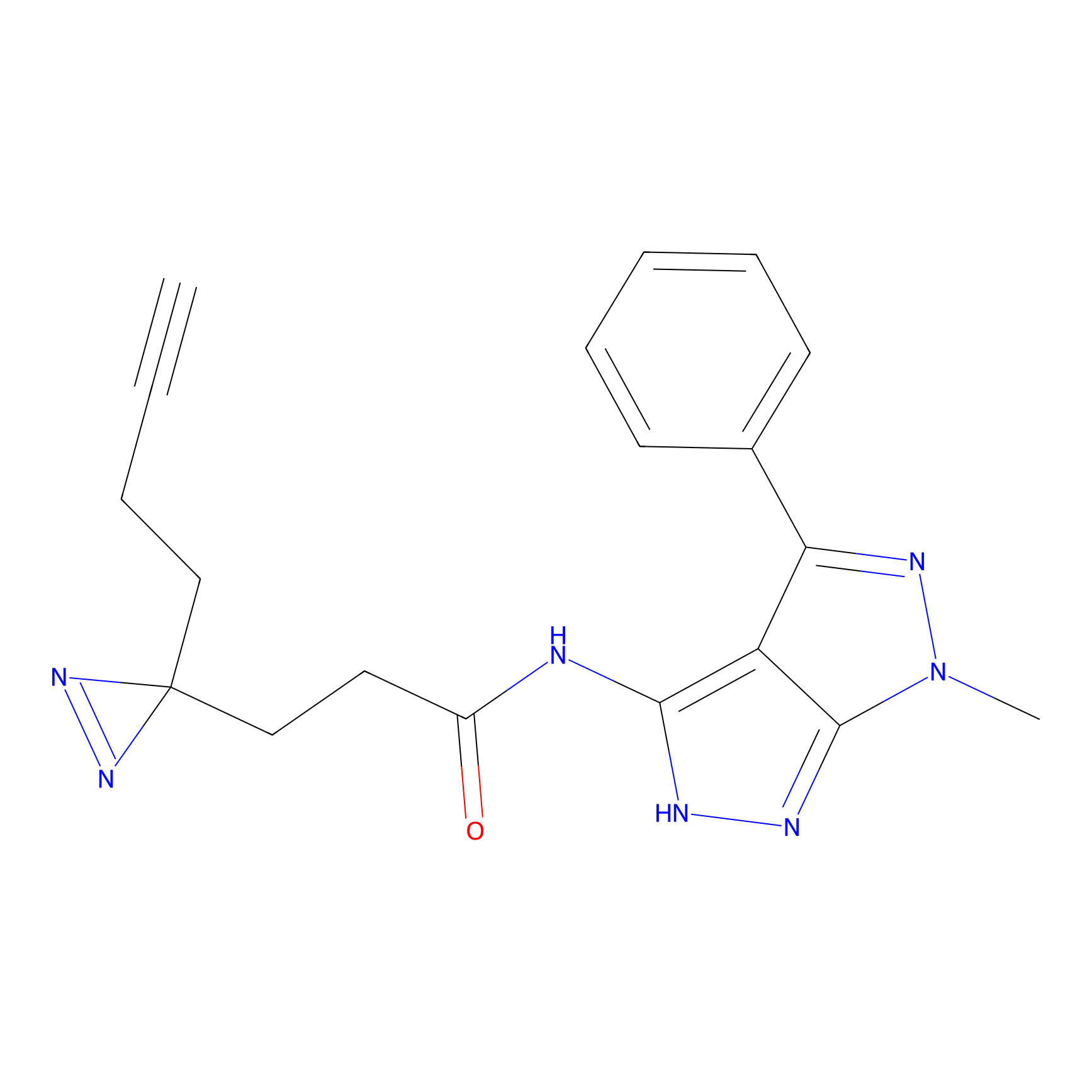
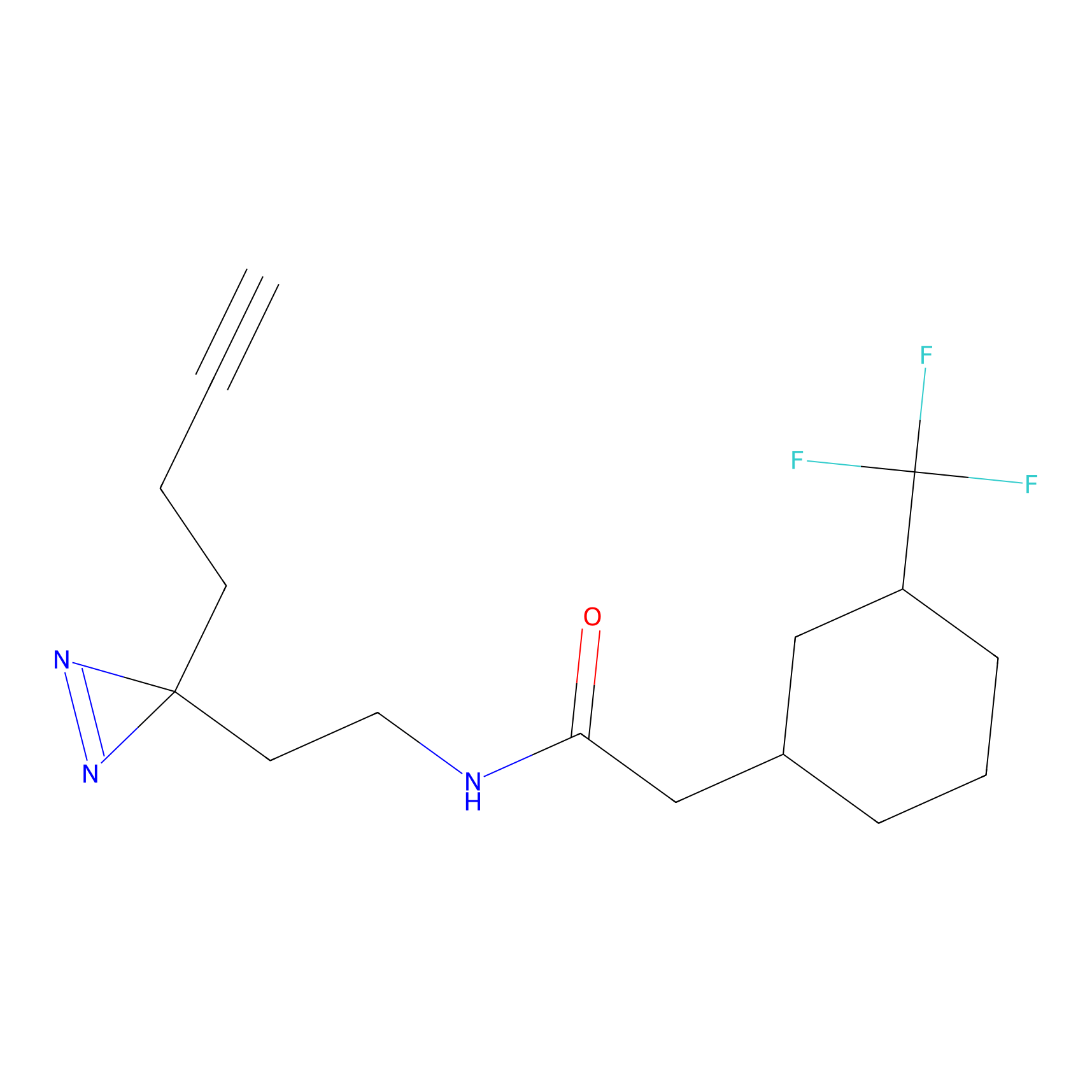
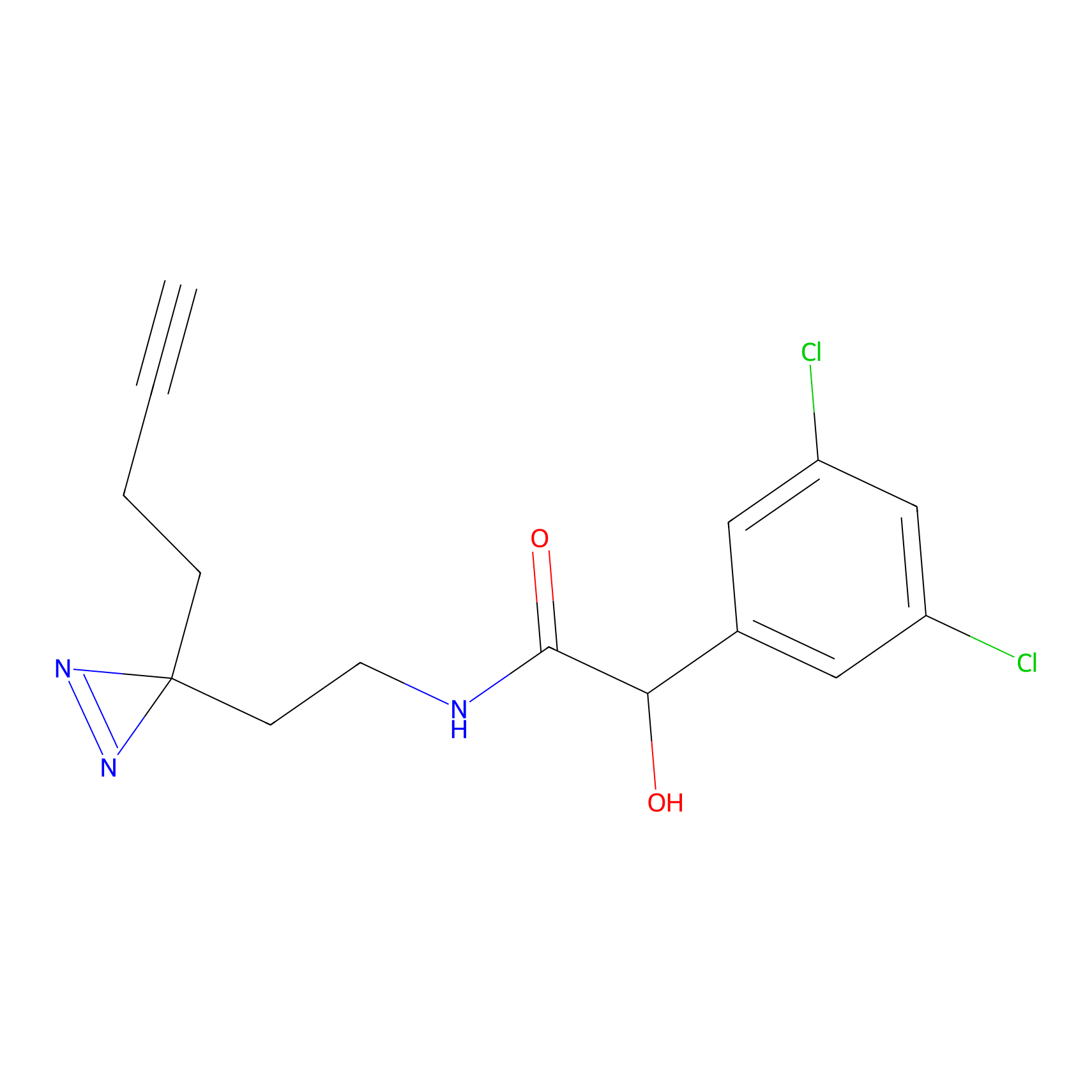
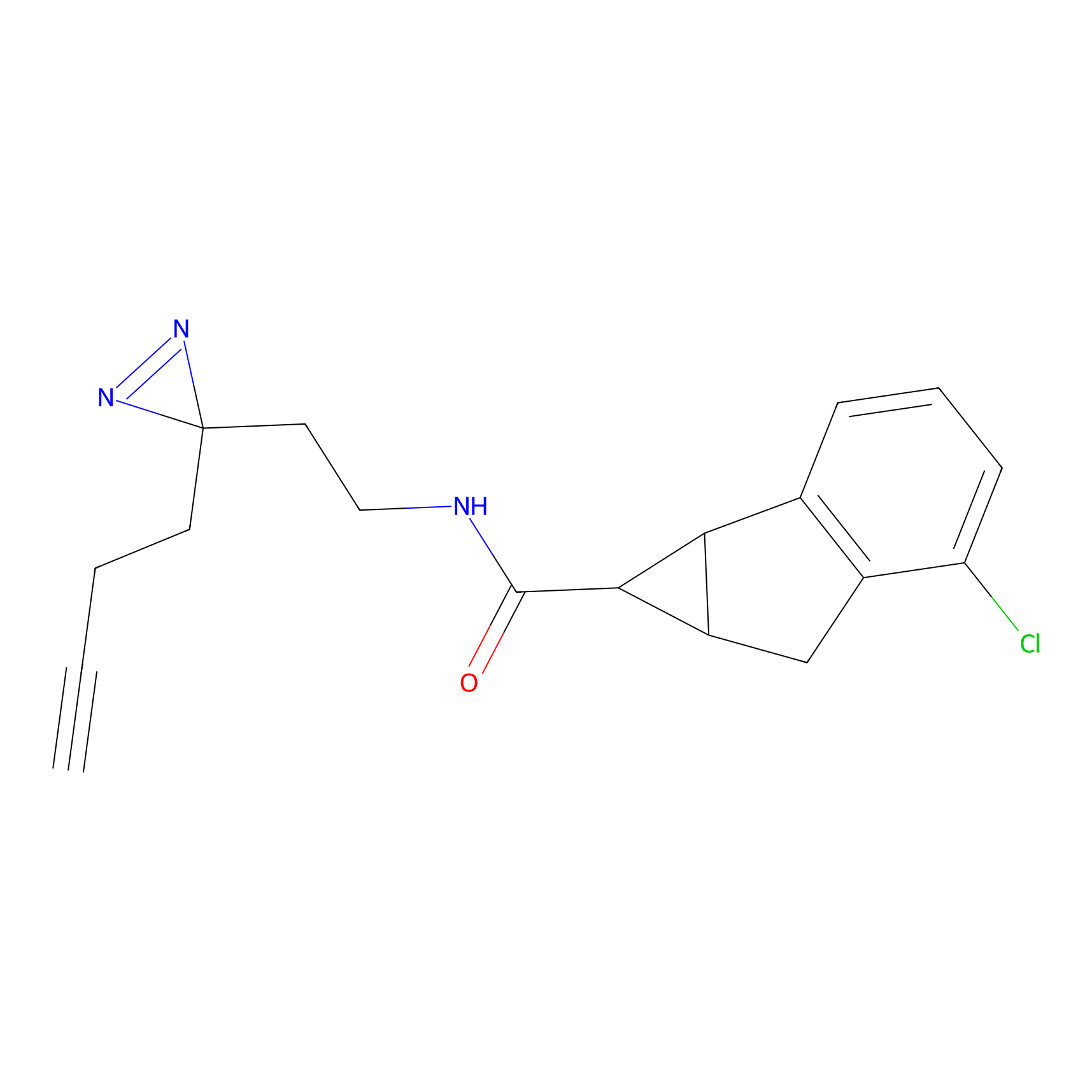
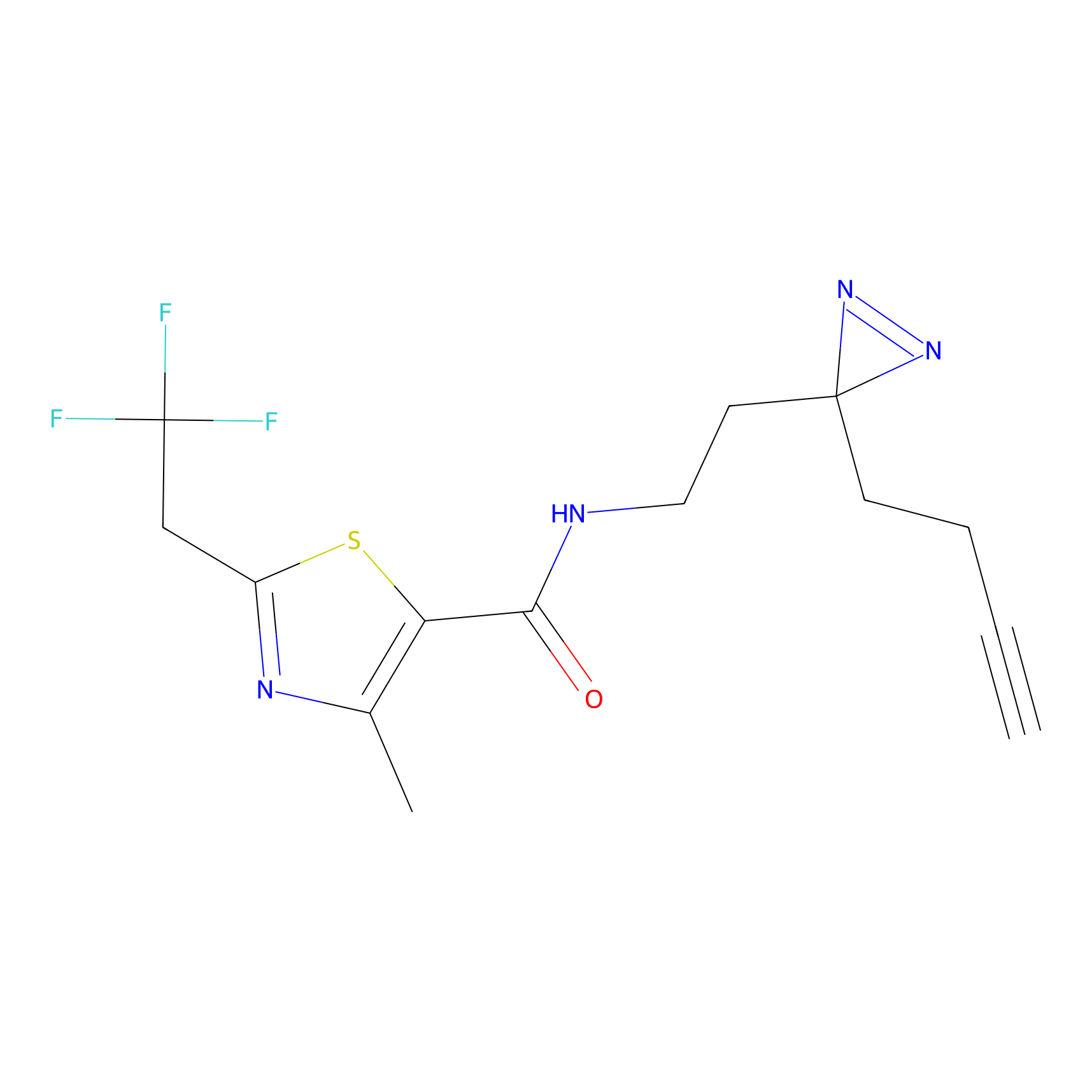
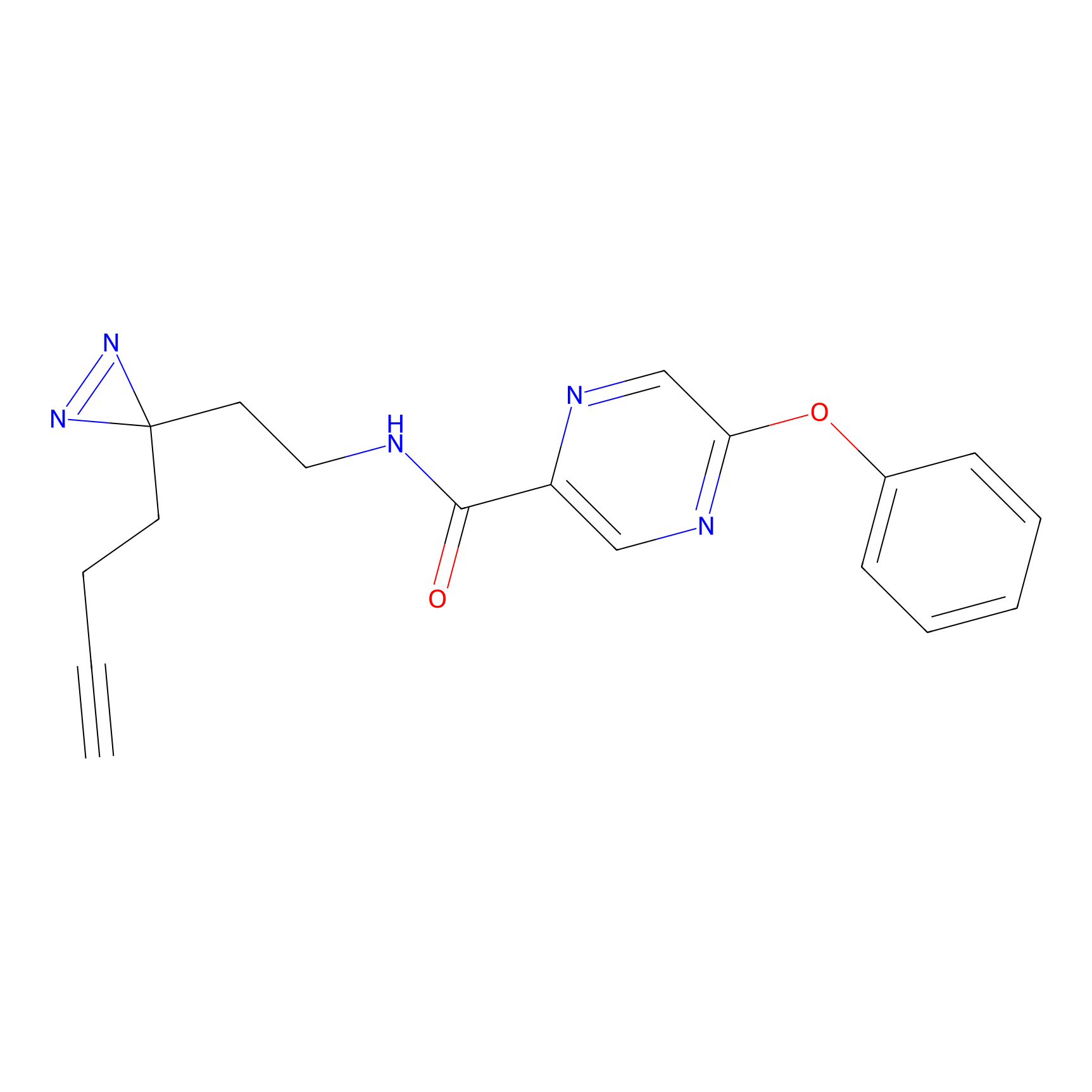
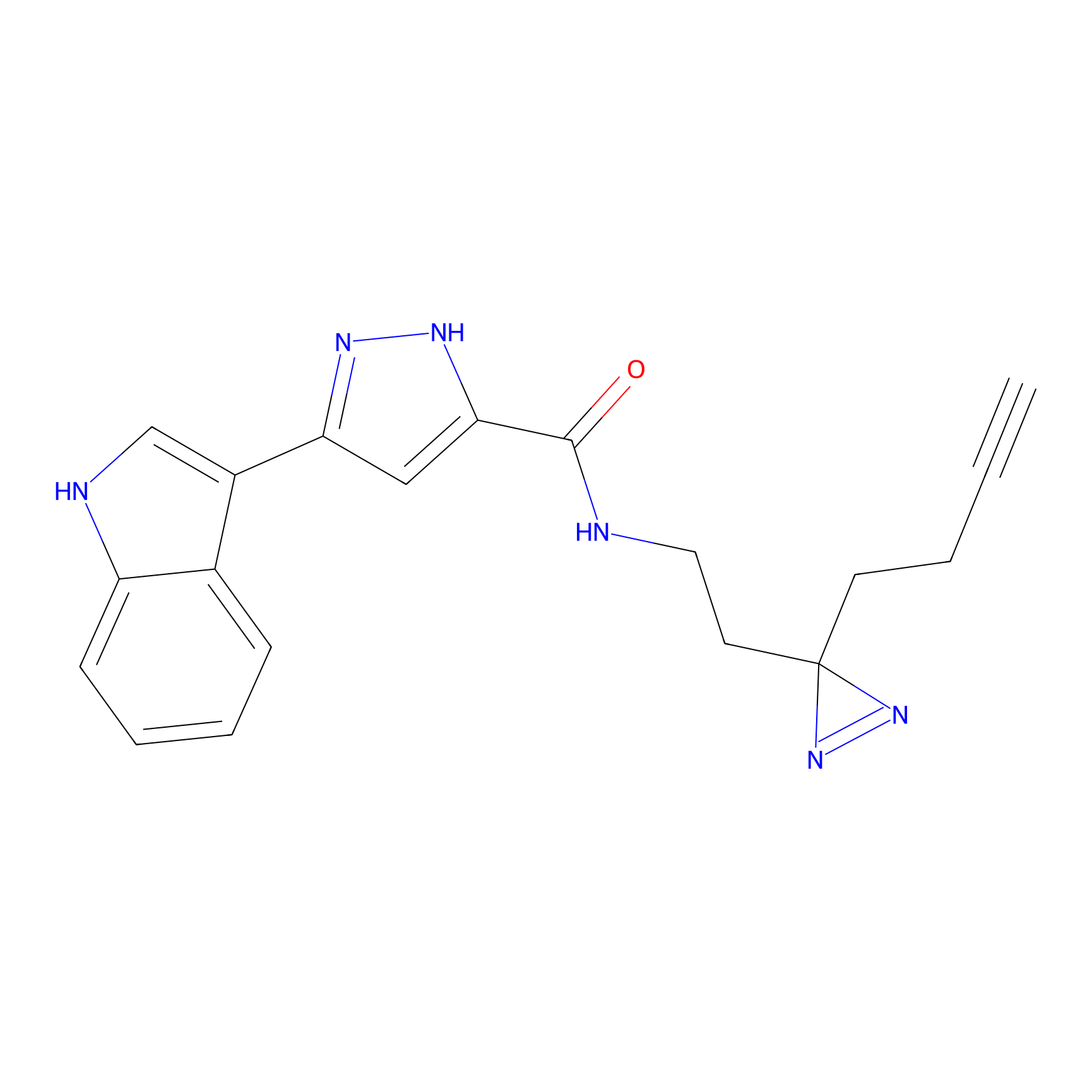
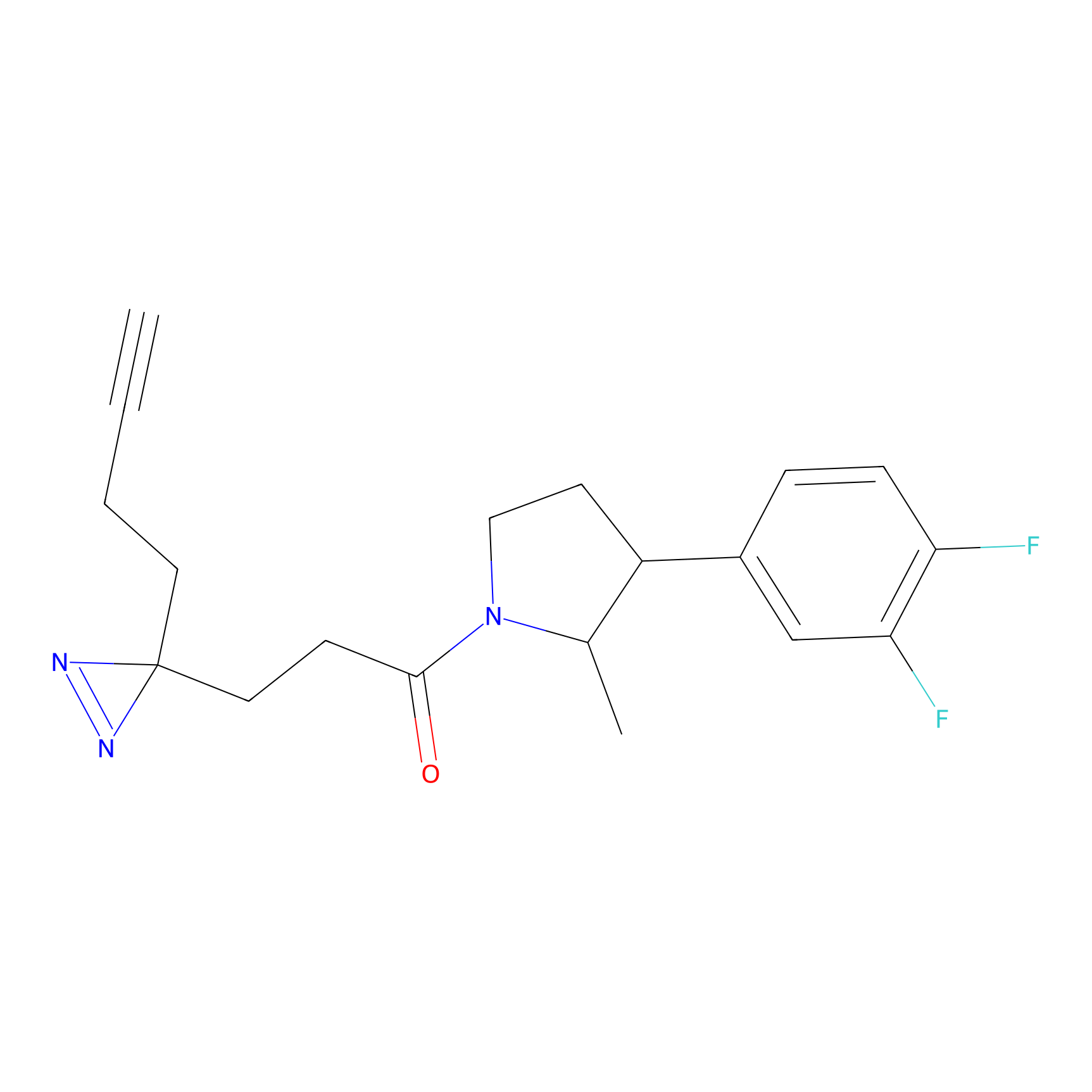
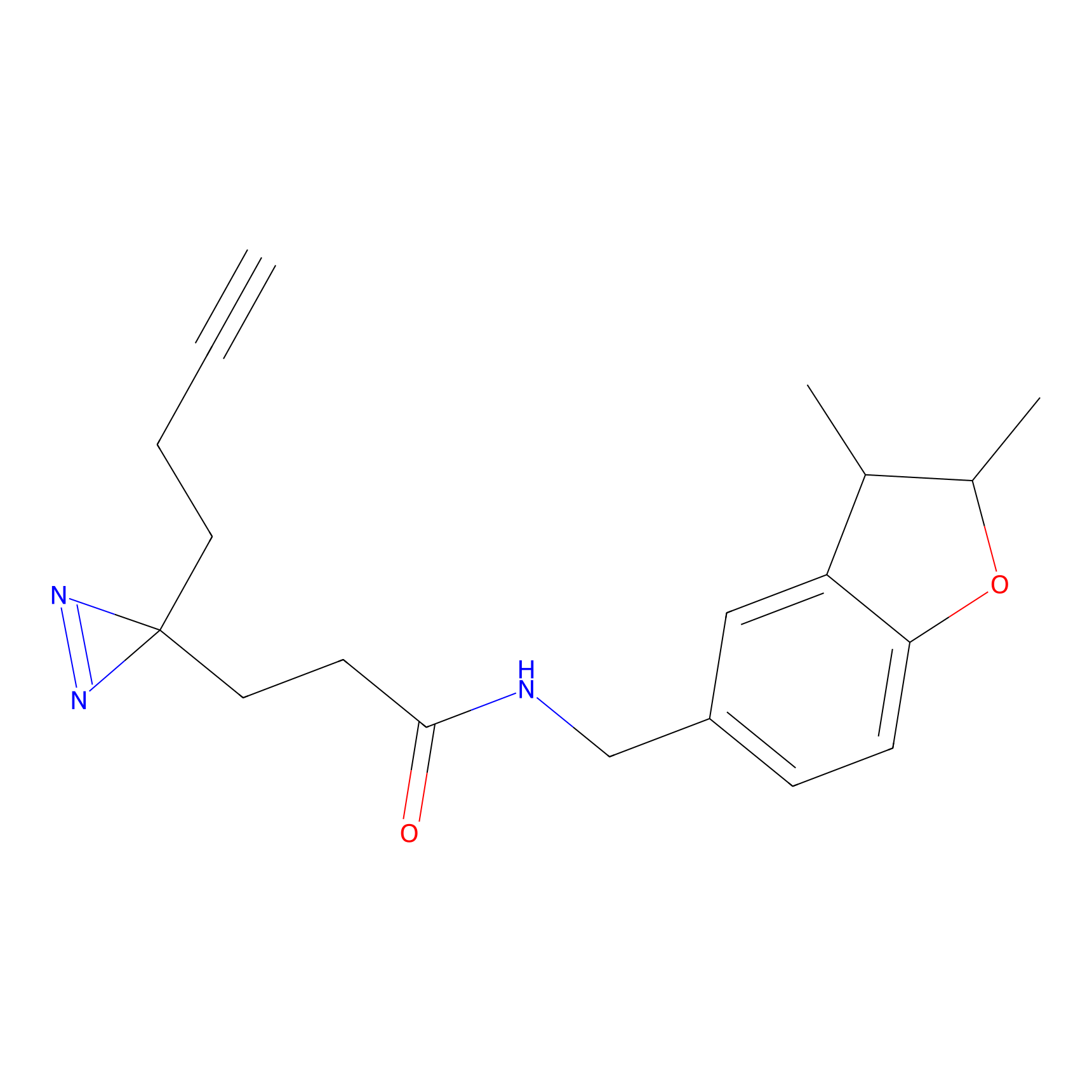
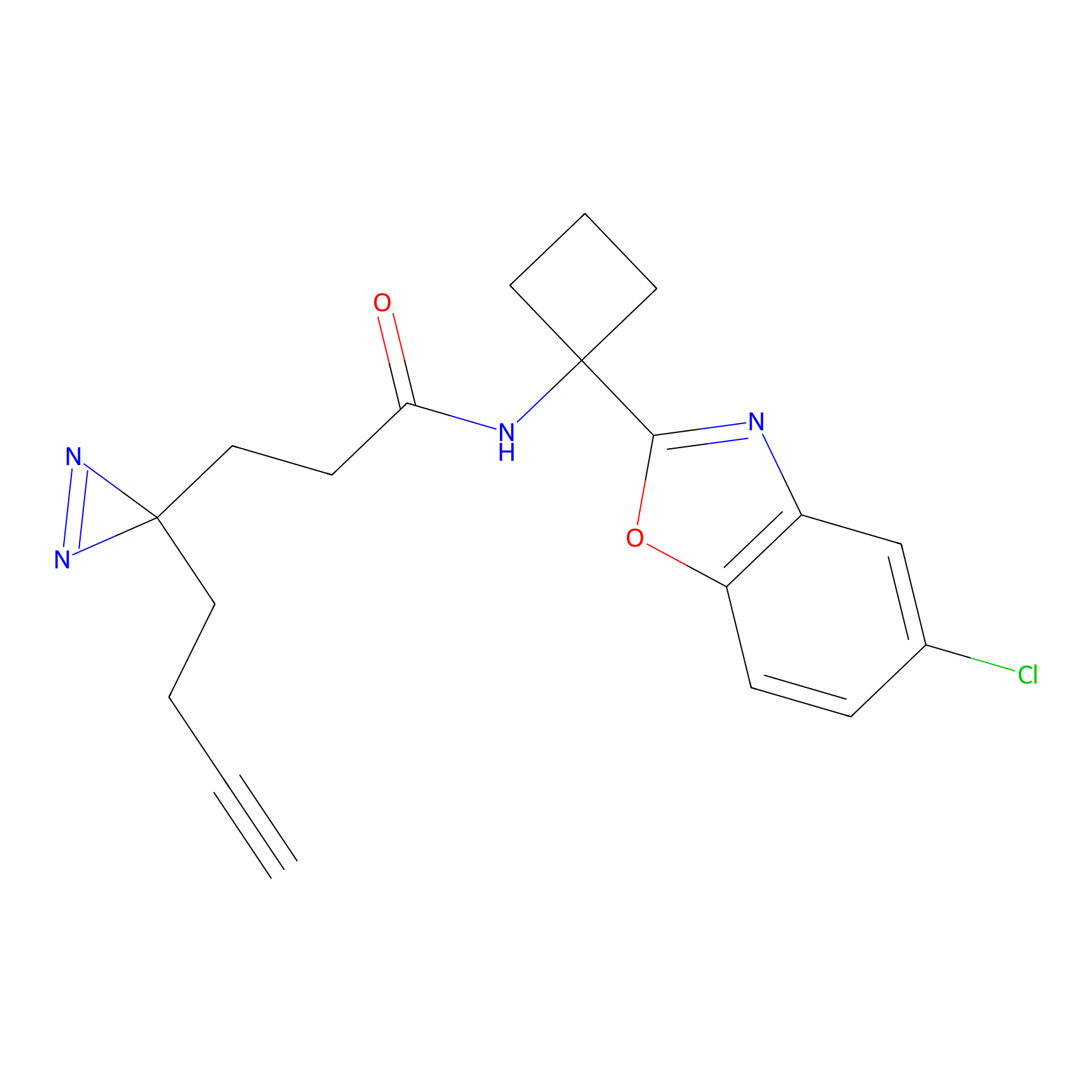
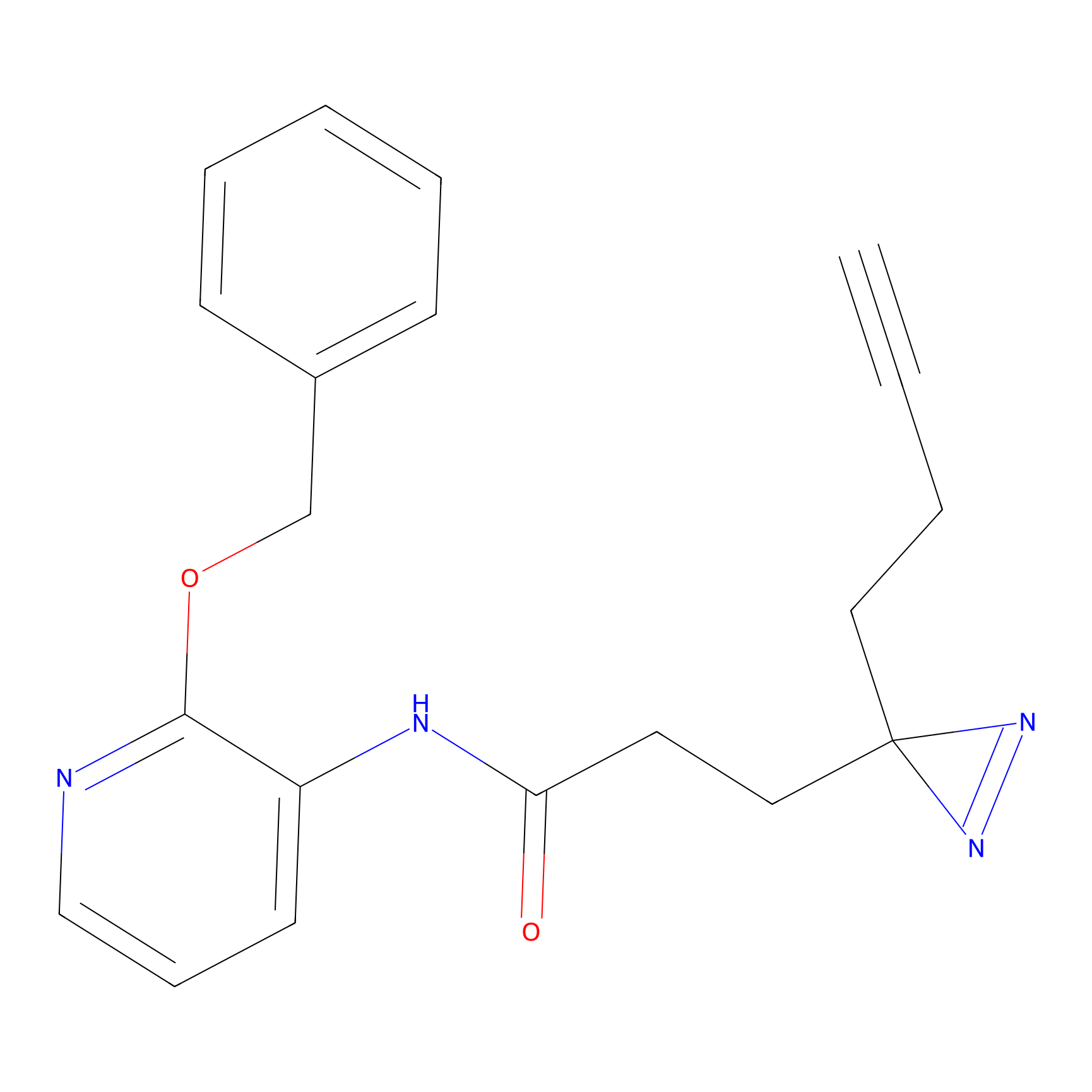
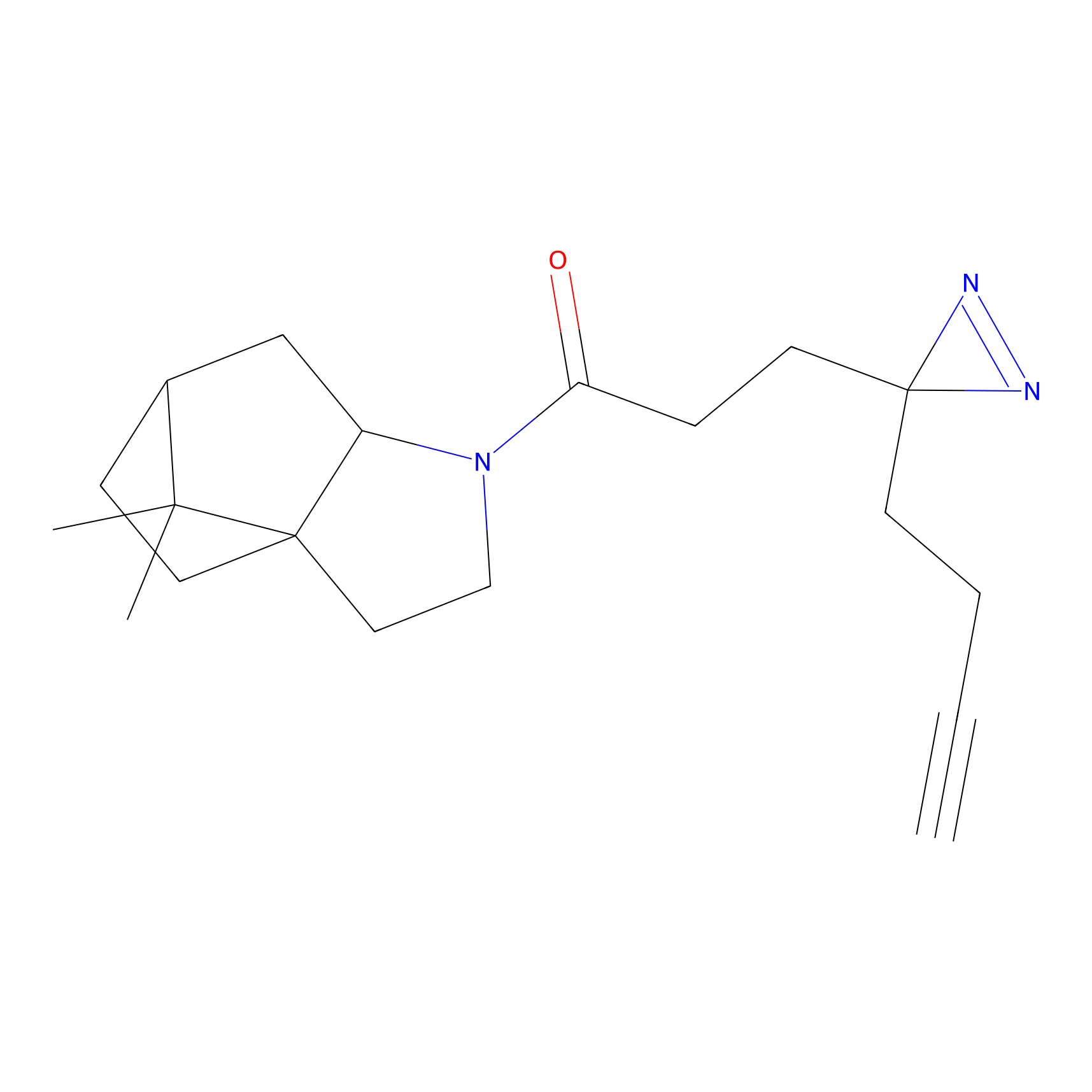
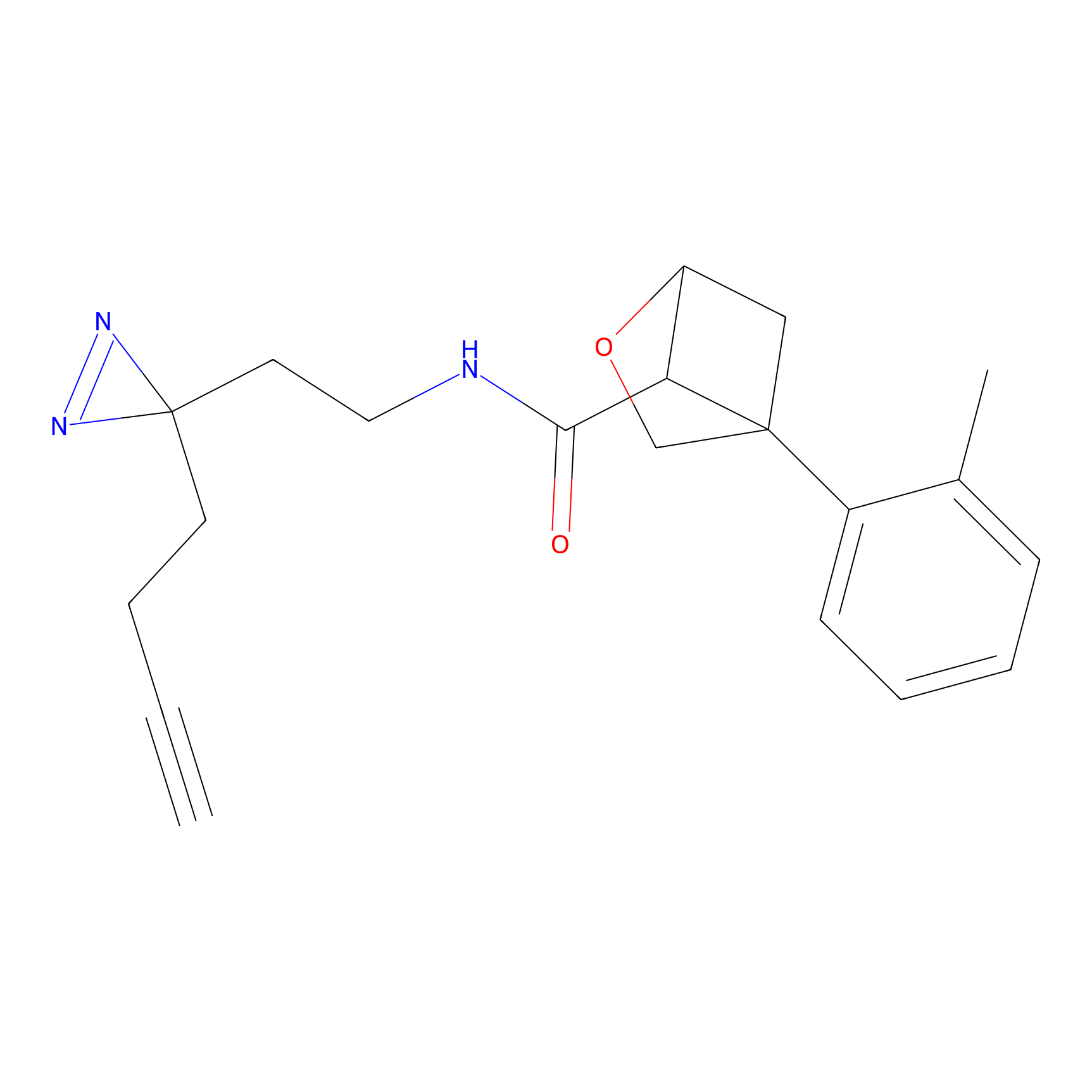
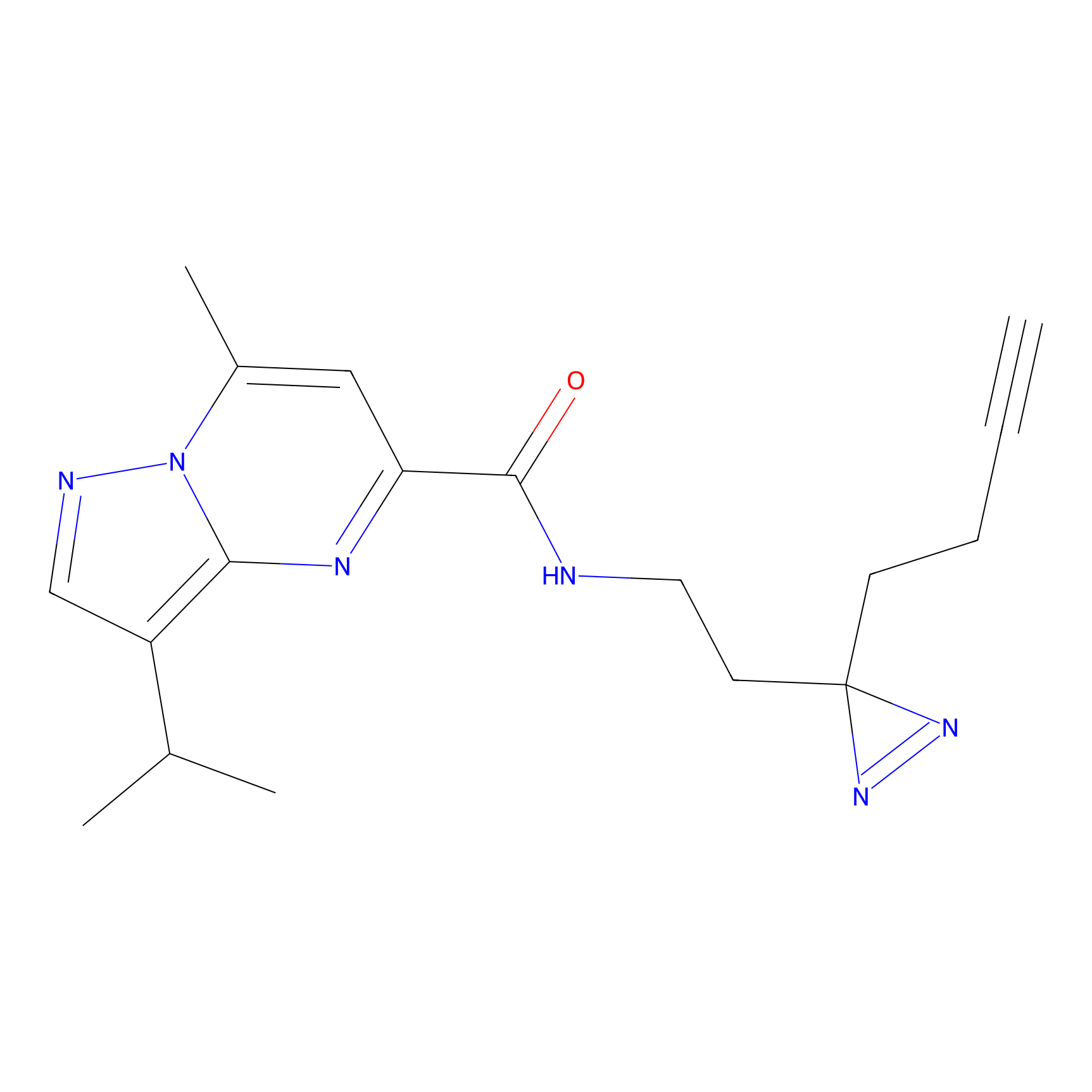
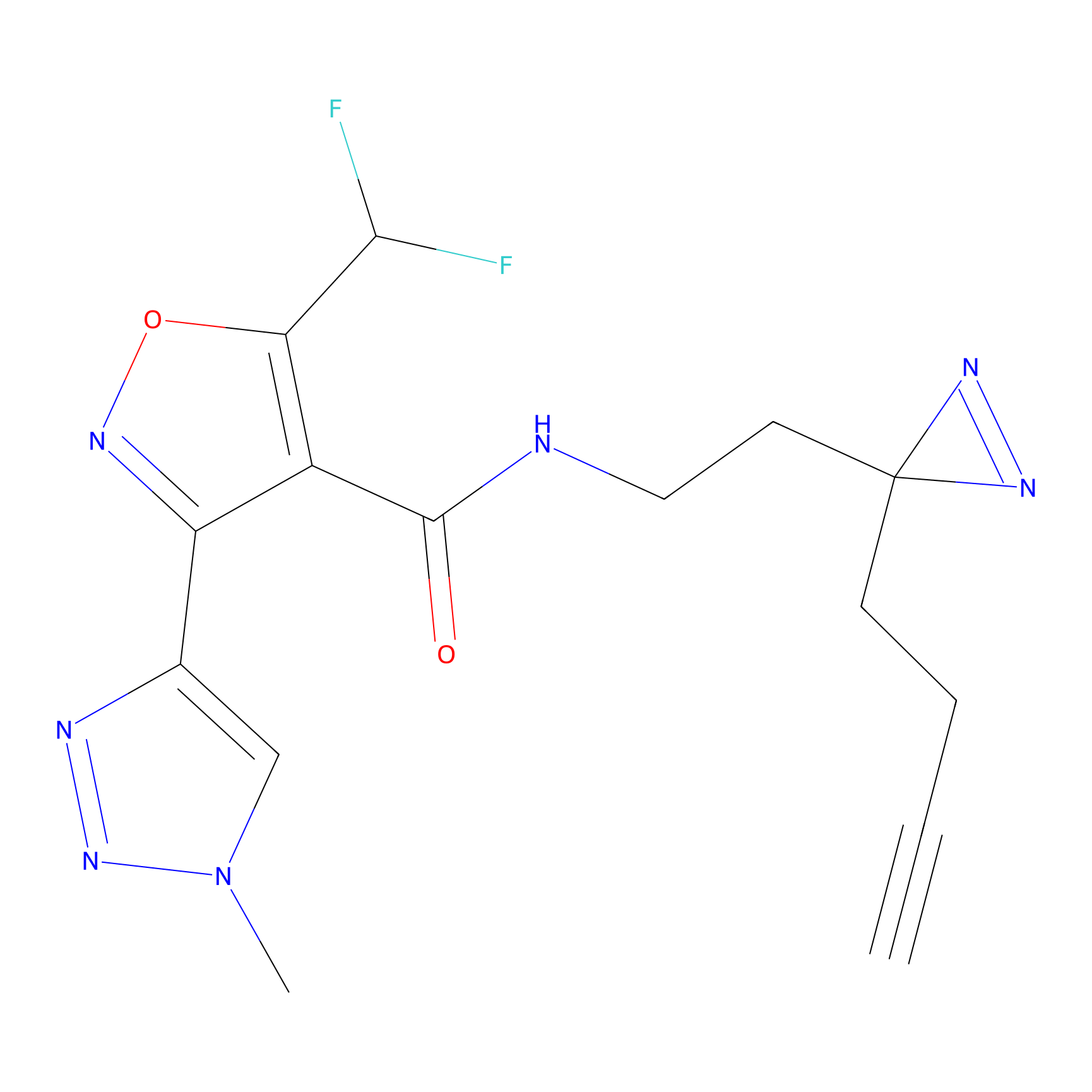
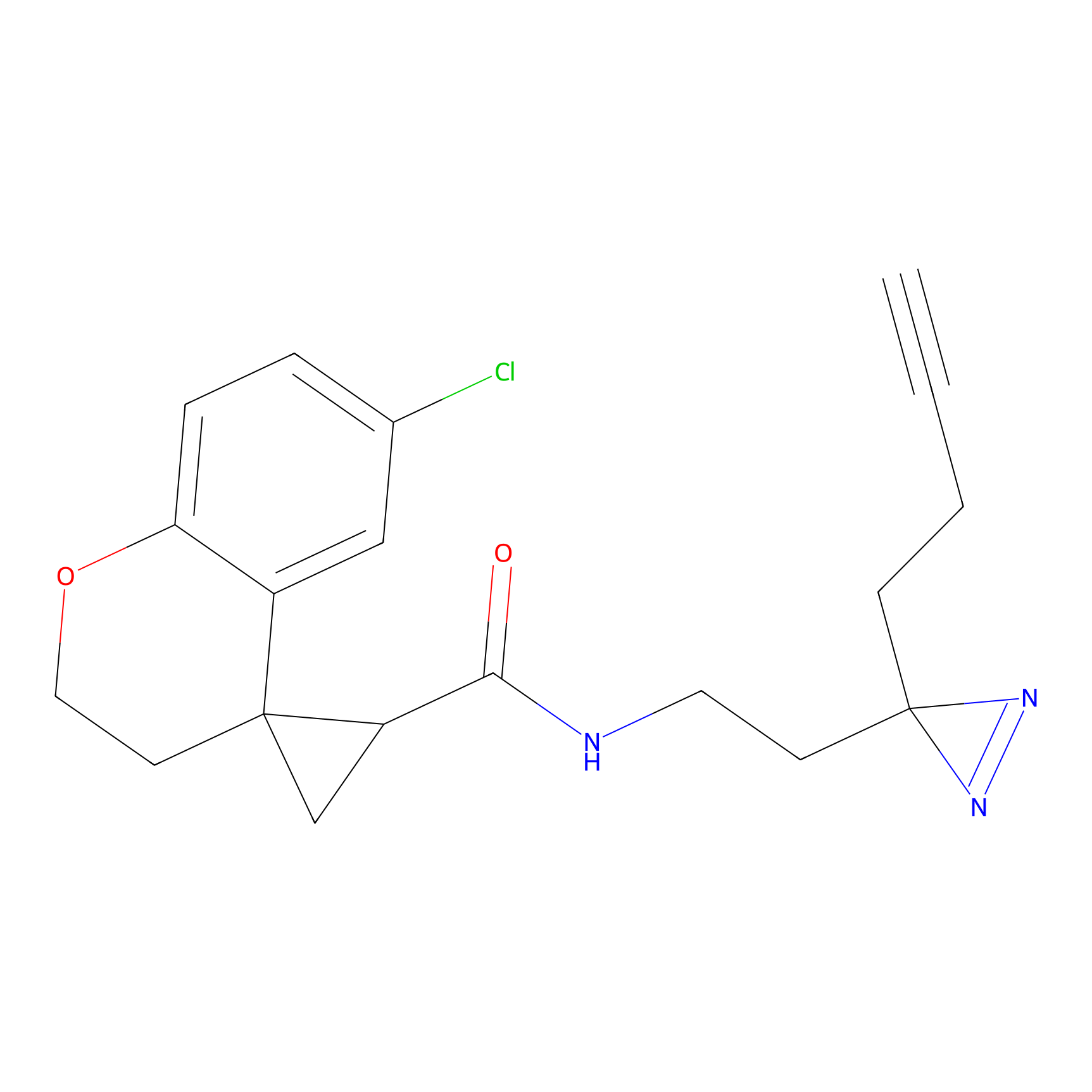
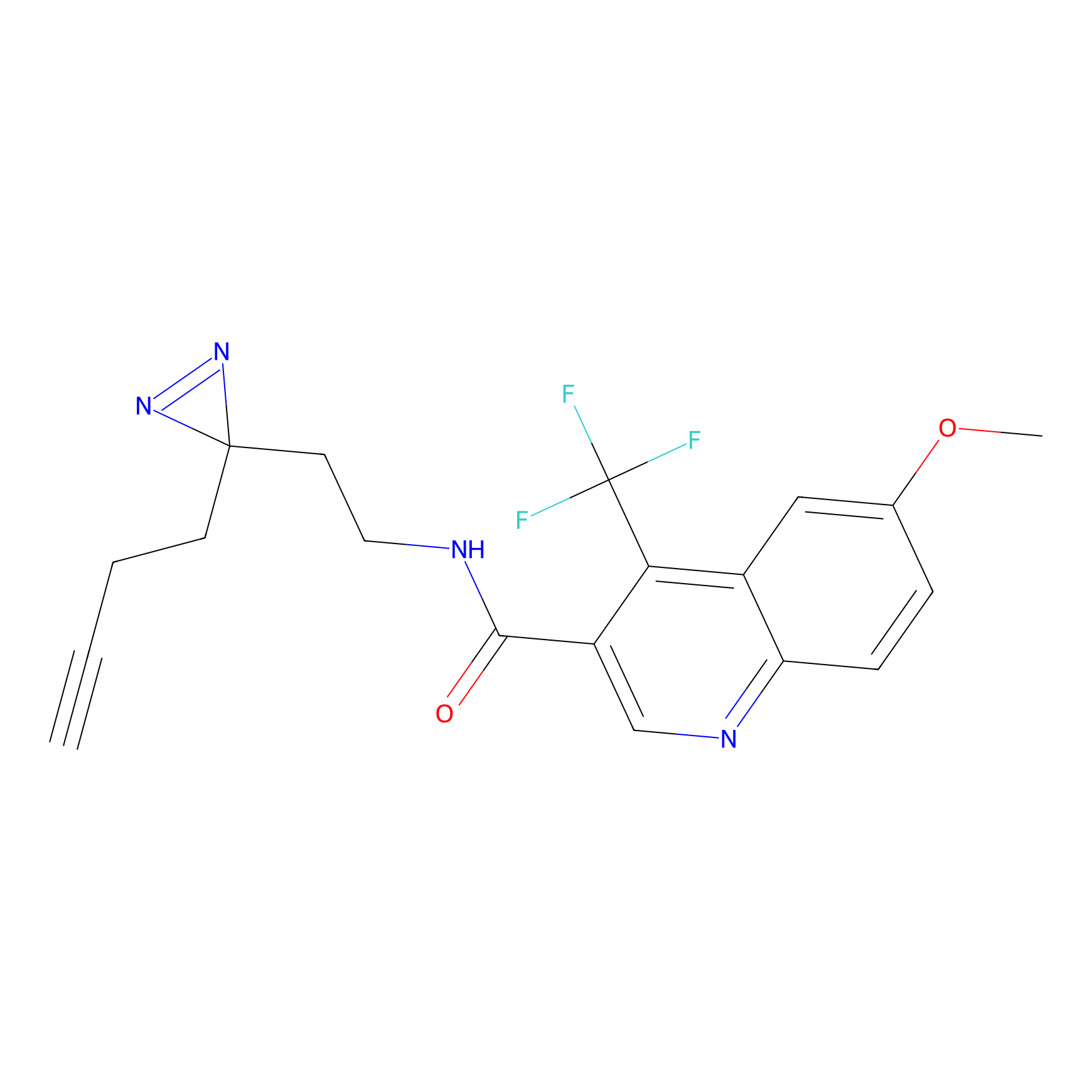
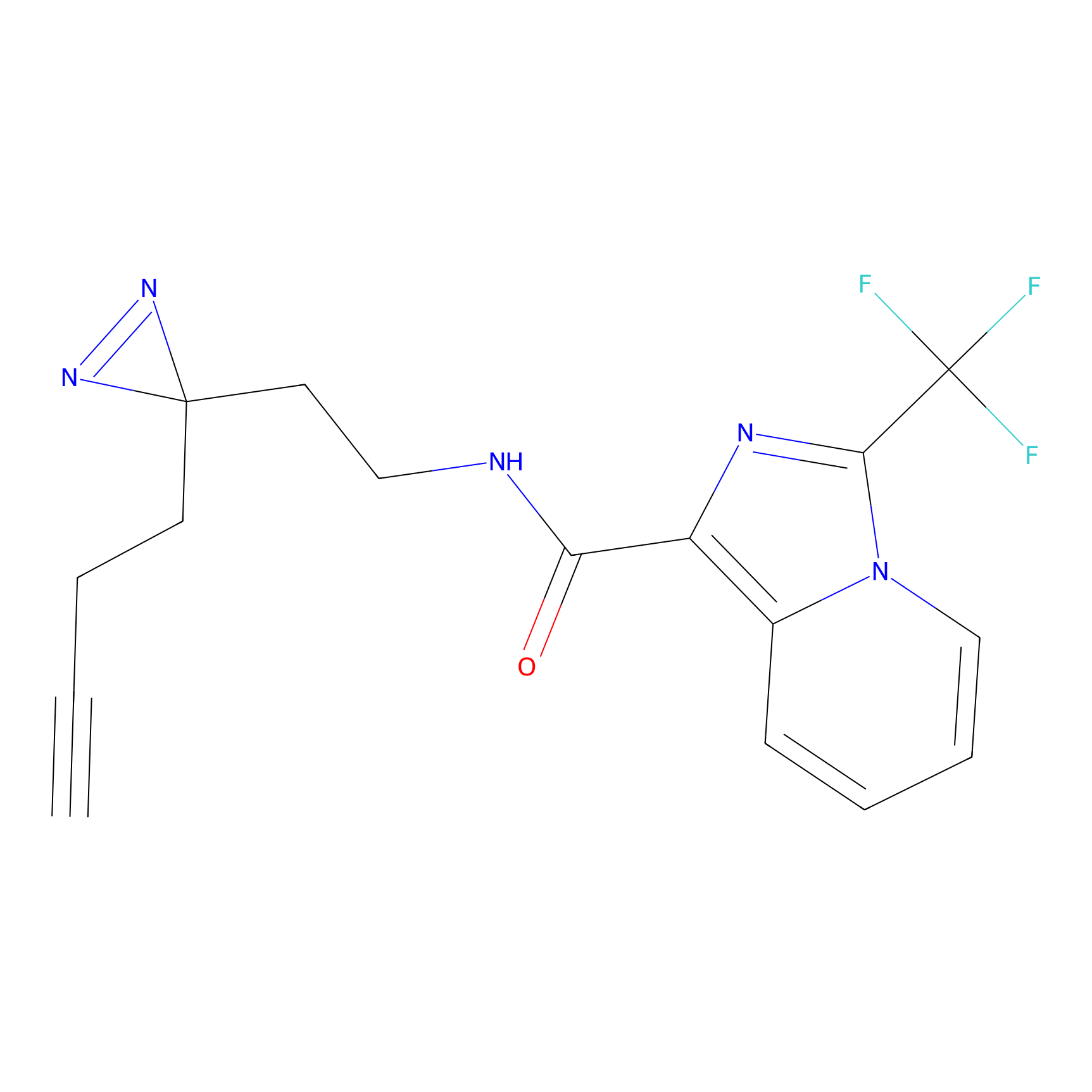
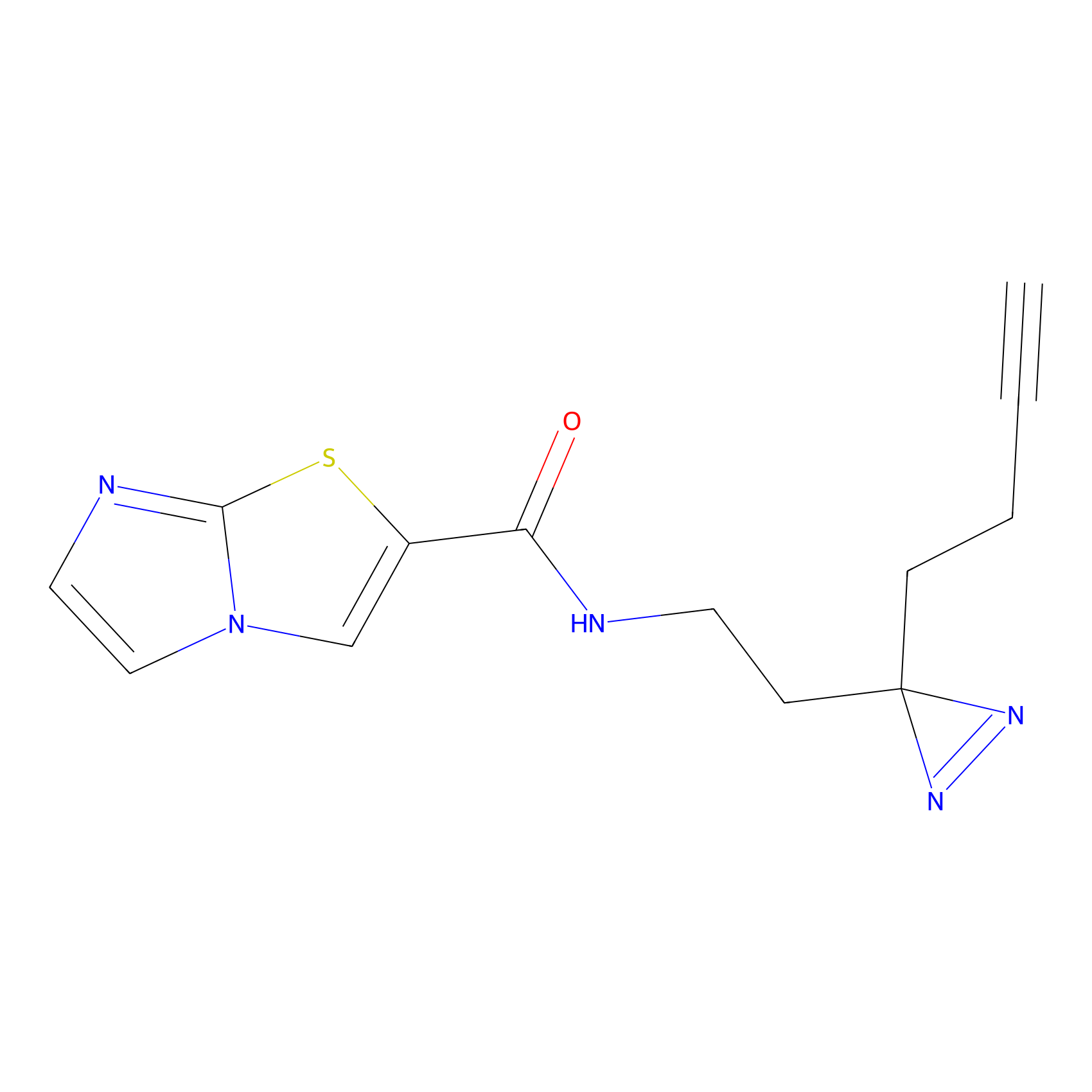
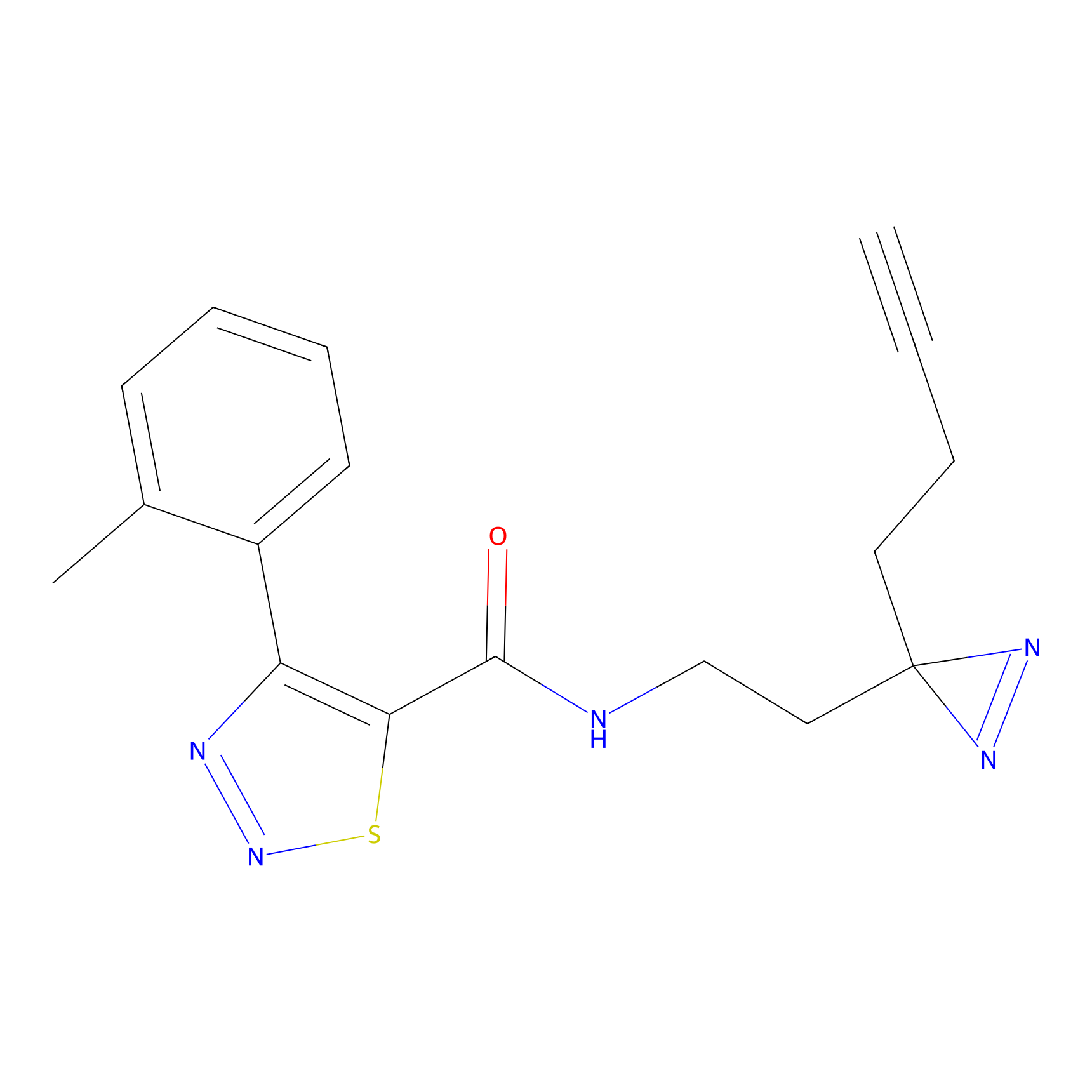
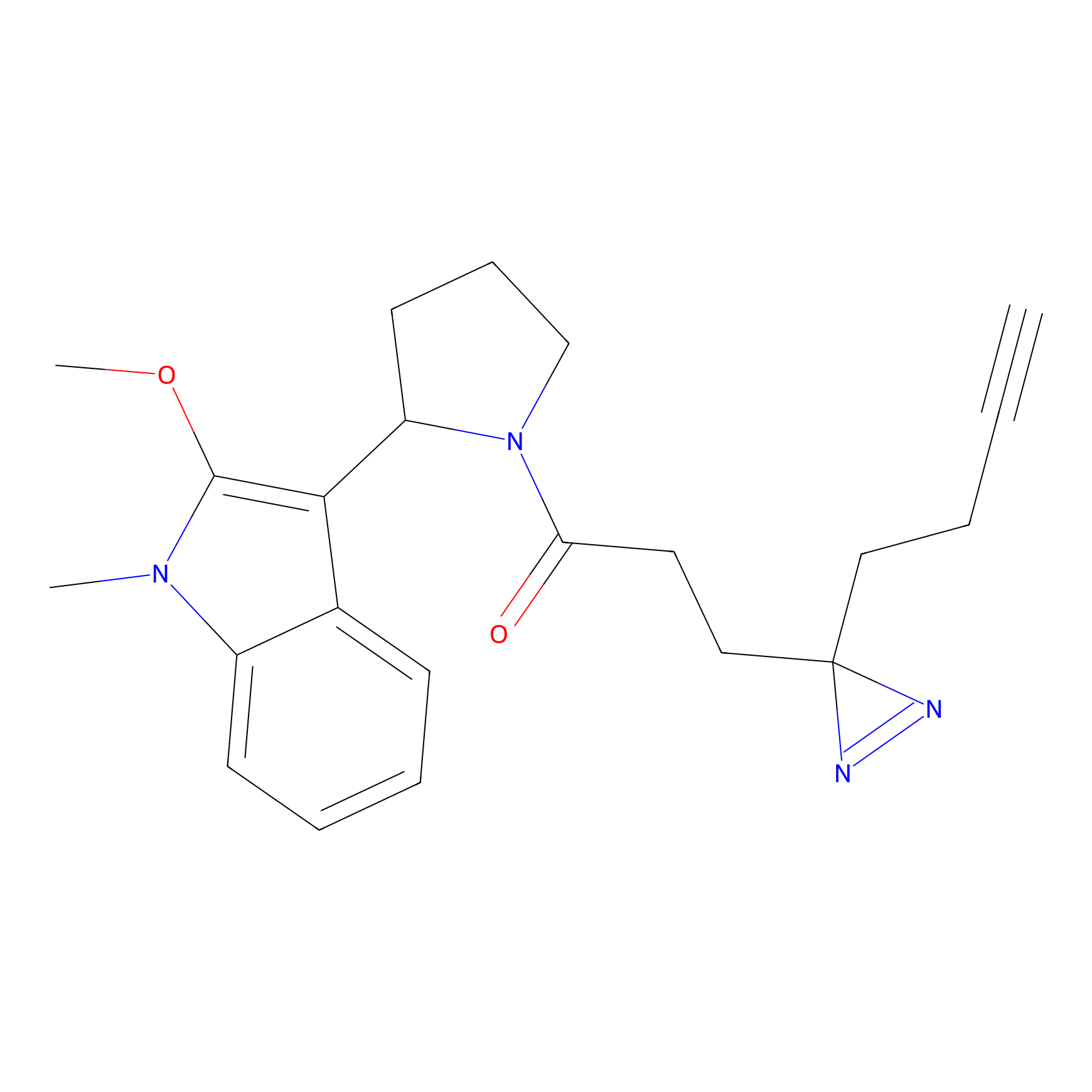
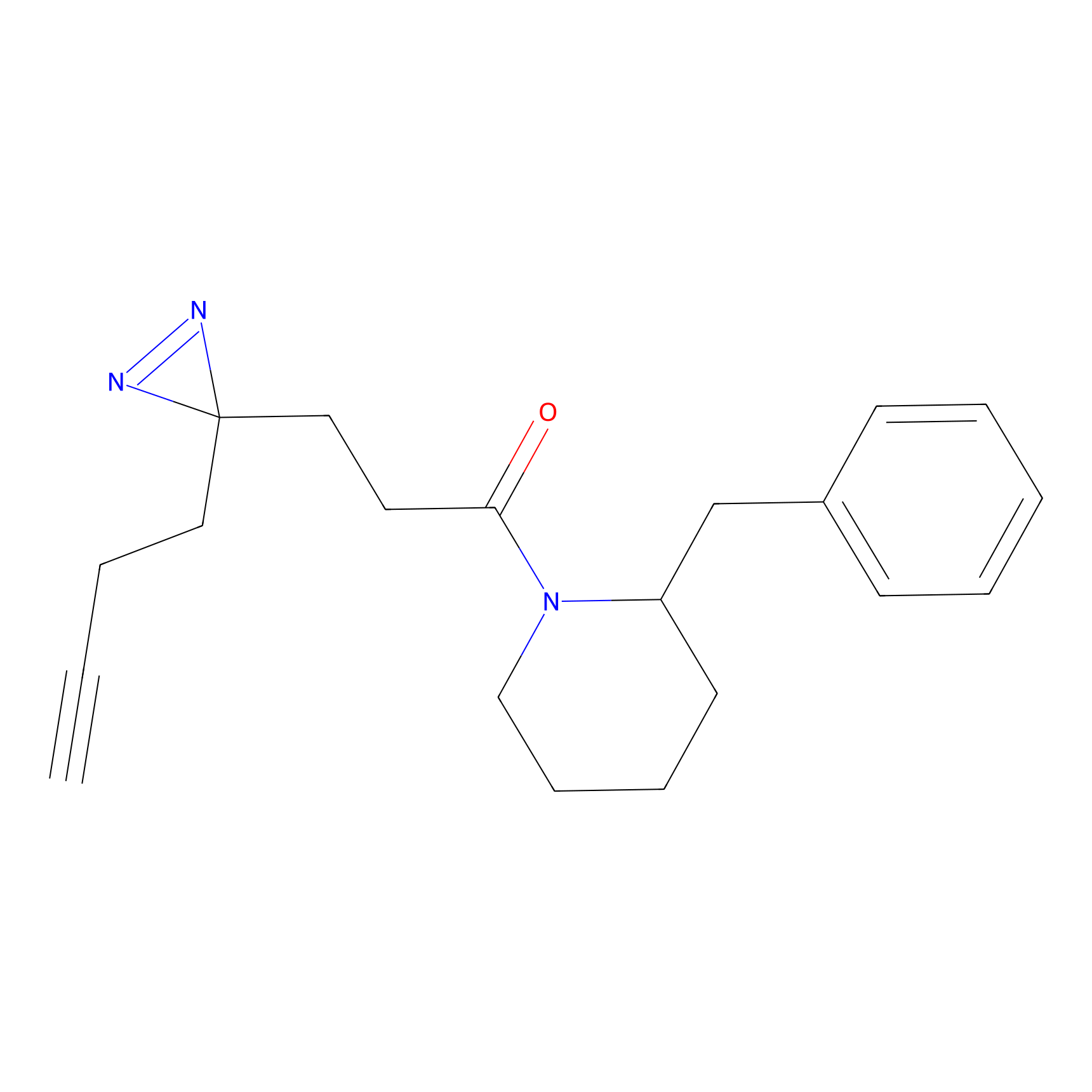
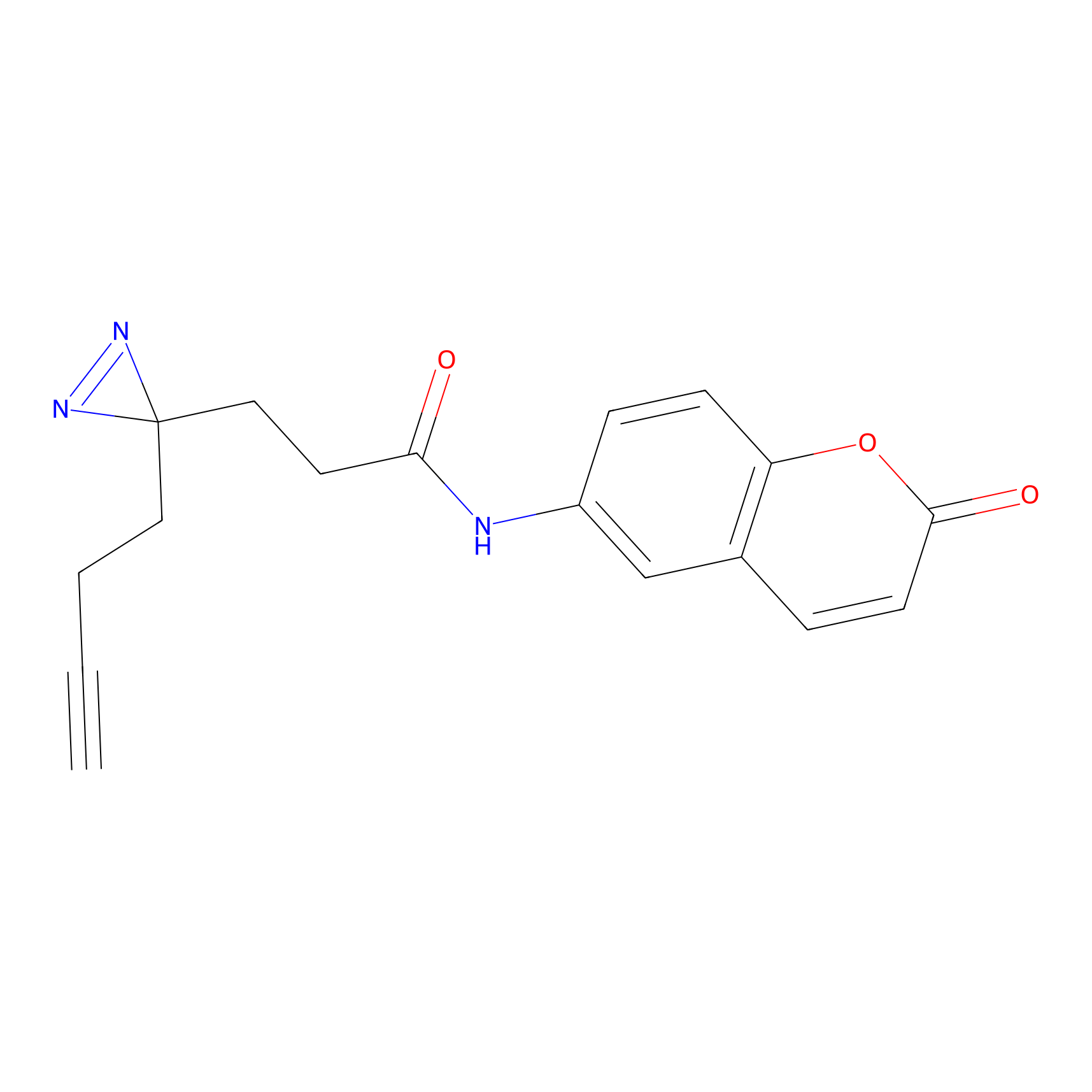
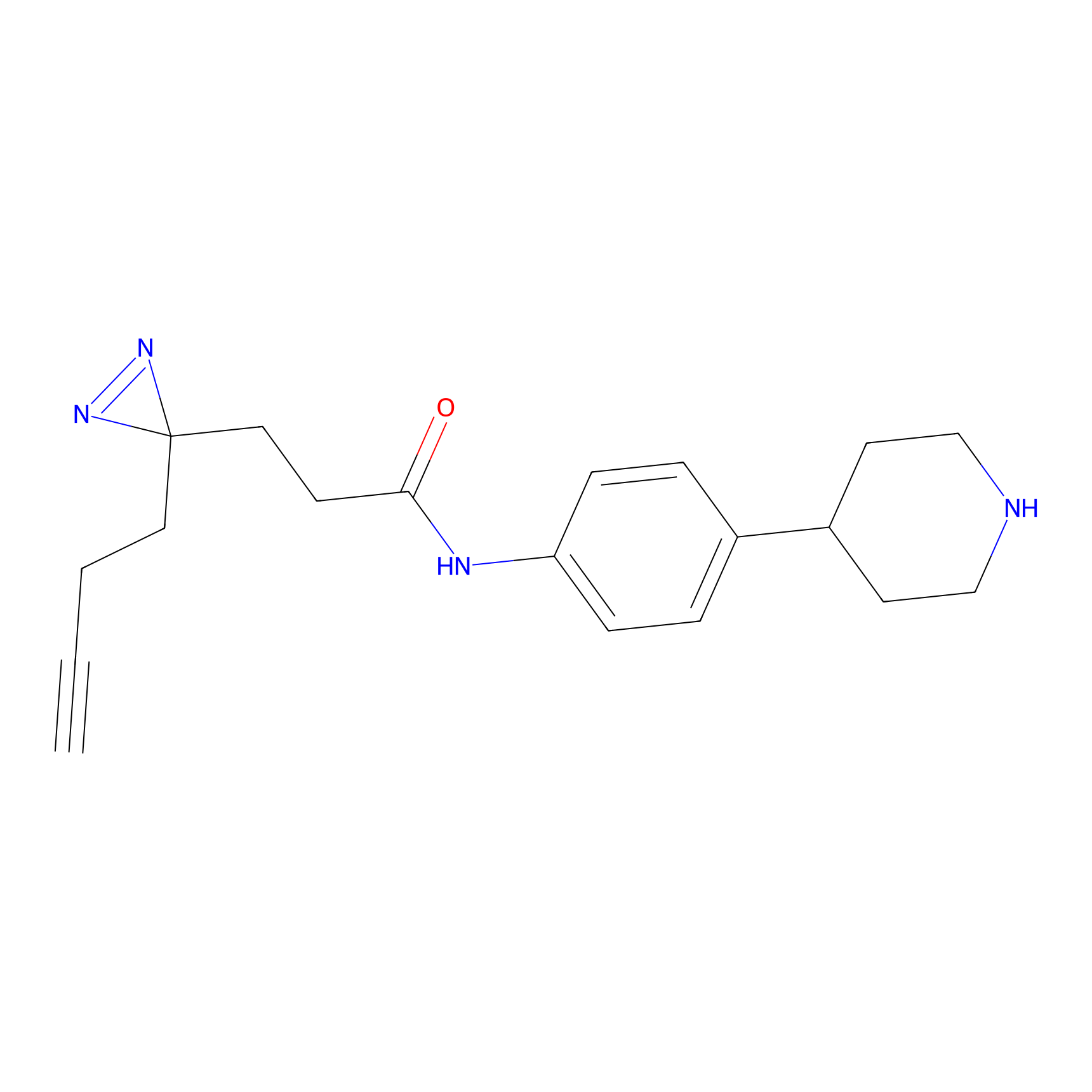
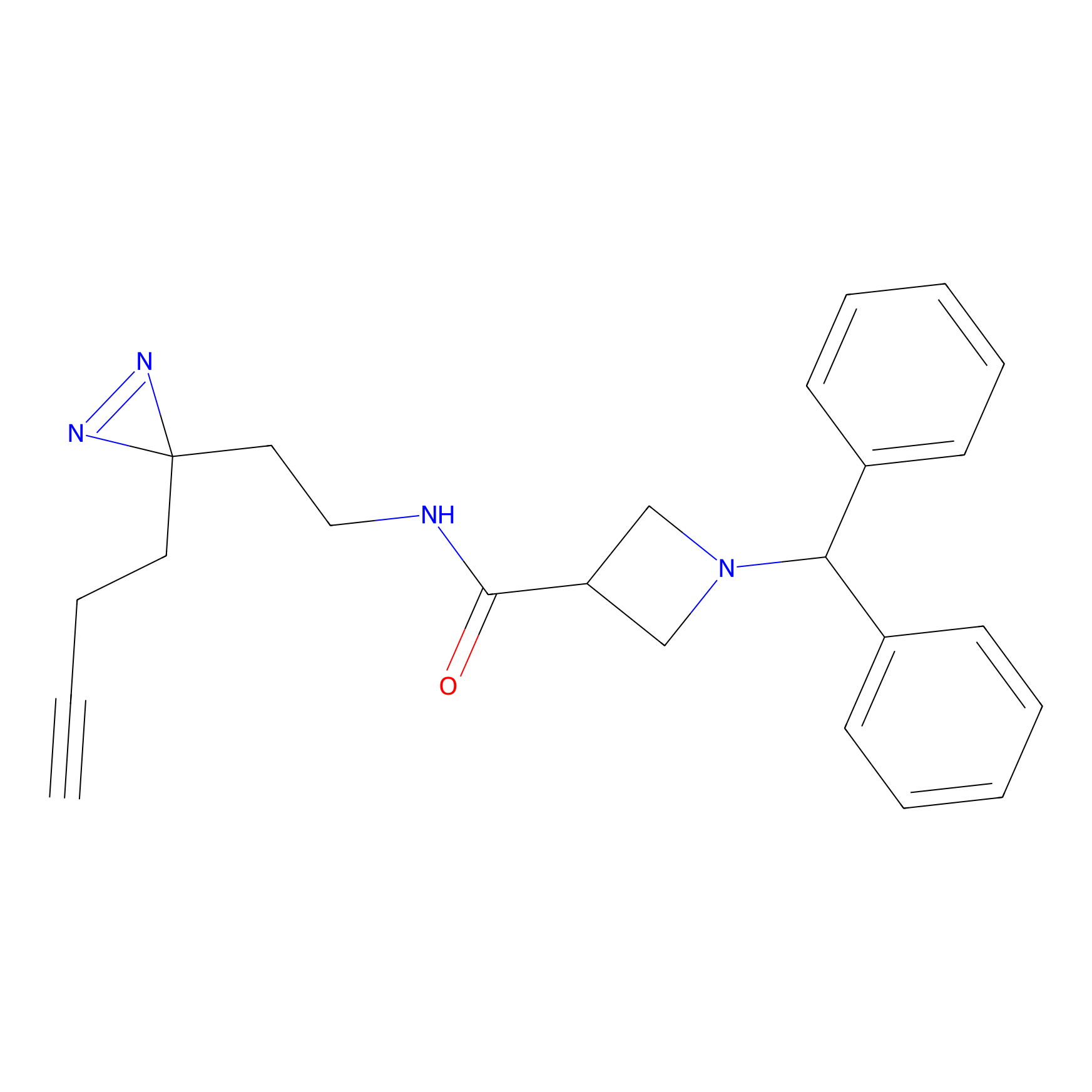
TH211 Probe Info |
 |
Y109(20.00); Y39(14.73); Y122(12.81); Y97(12.60) | LDD0257 | [2] | |
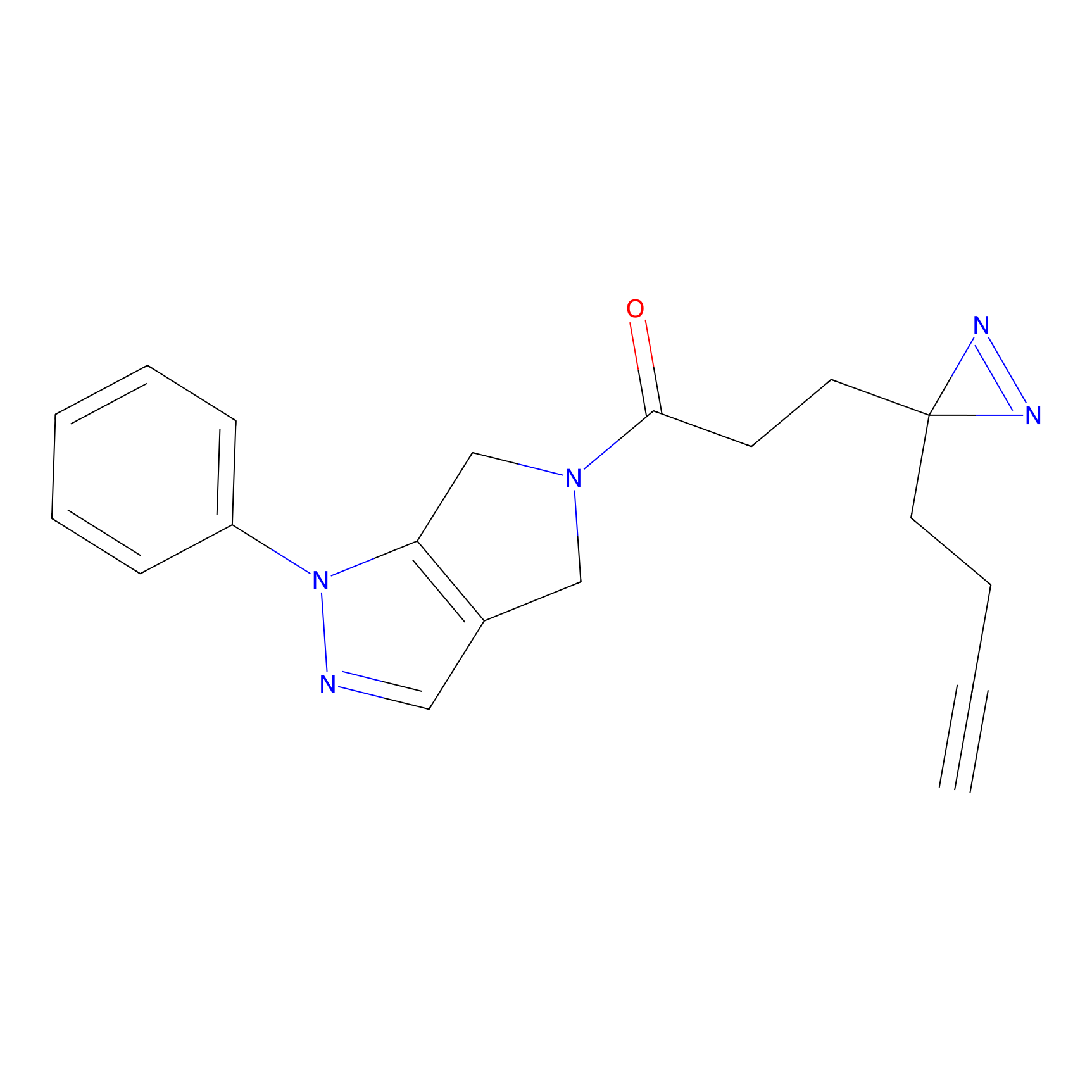
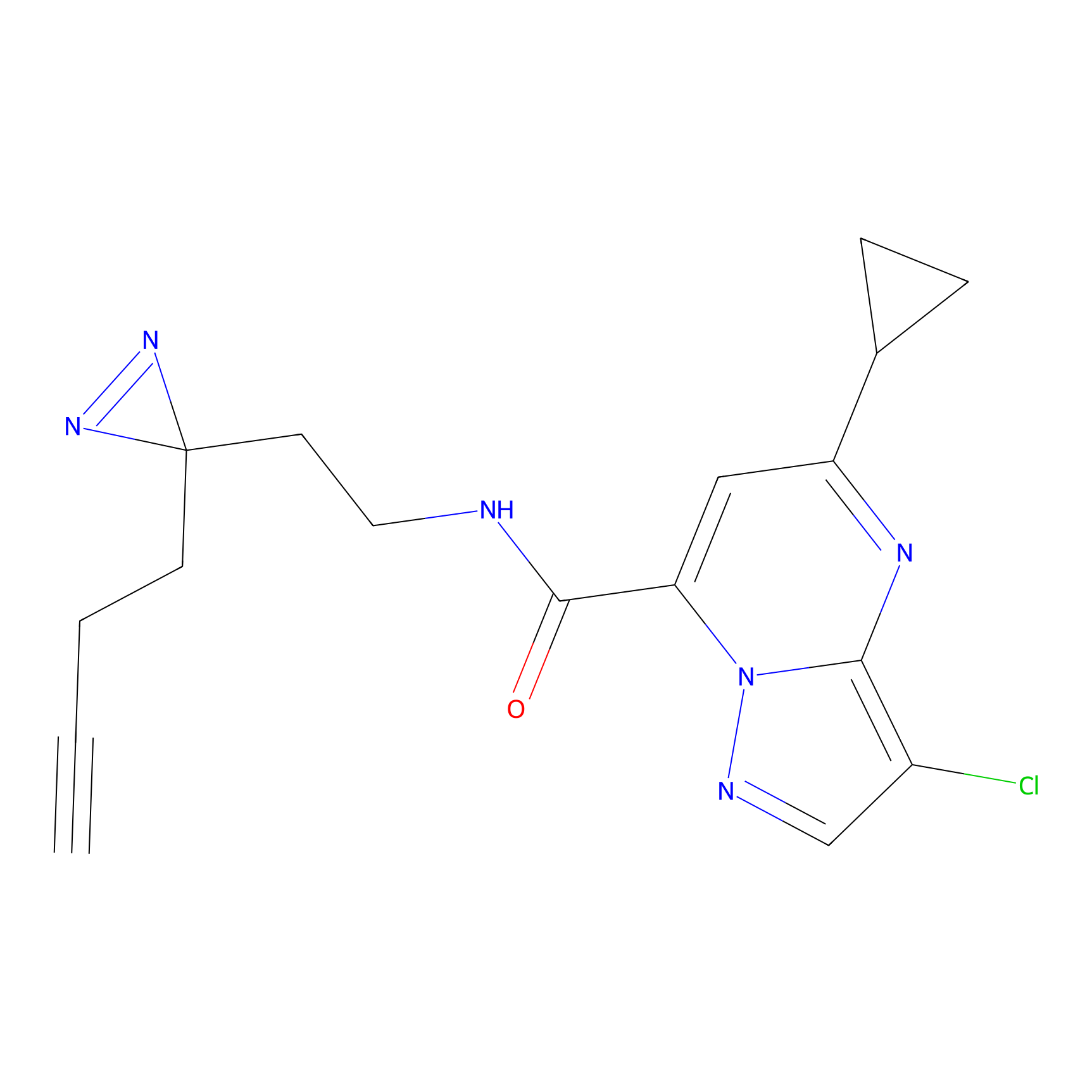
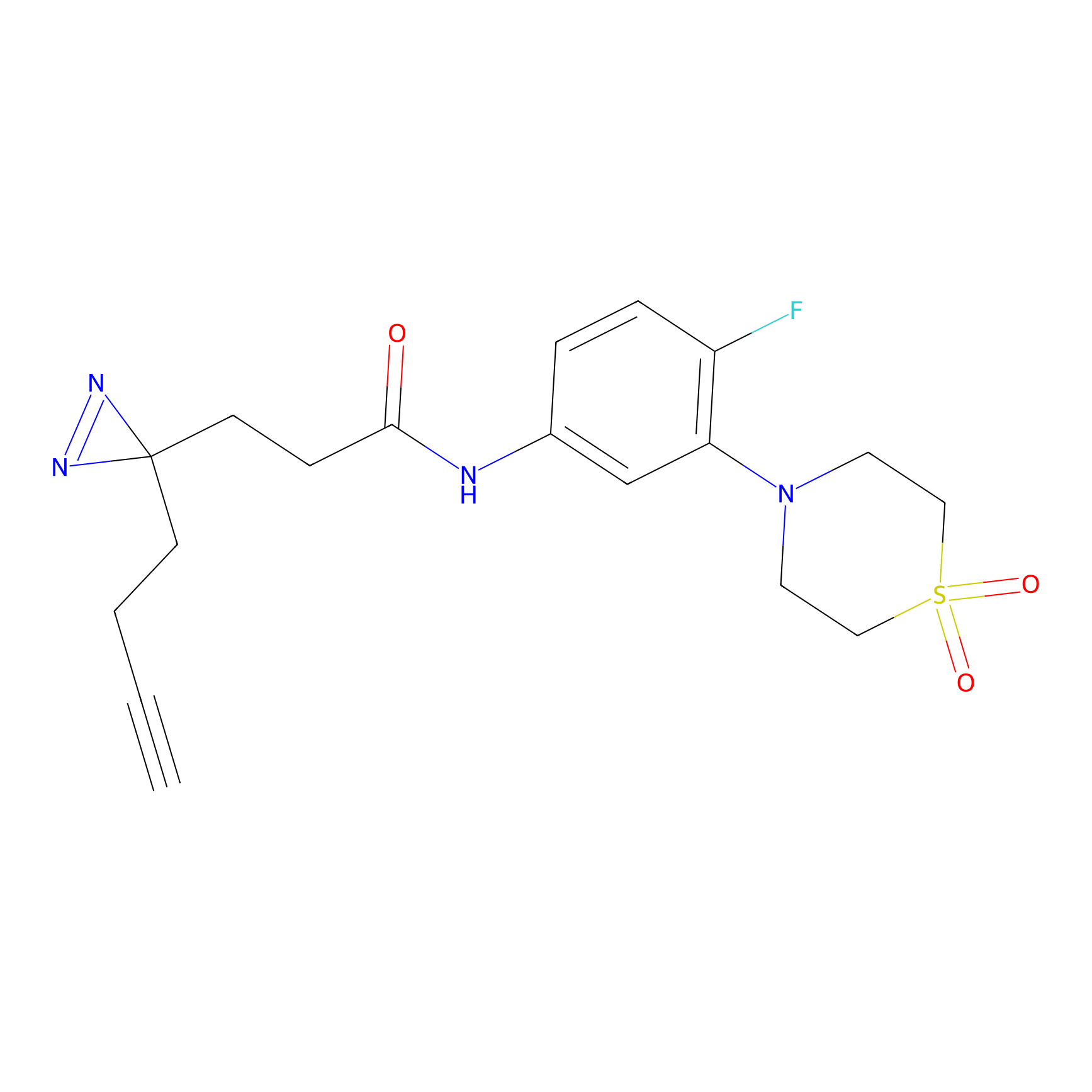
|
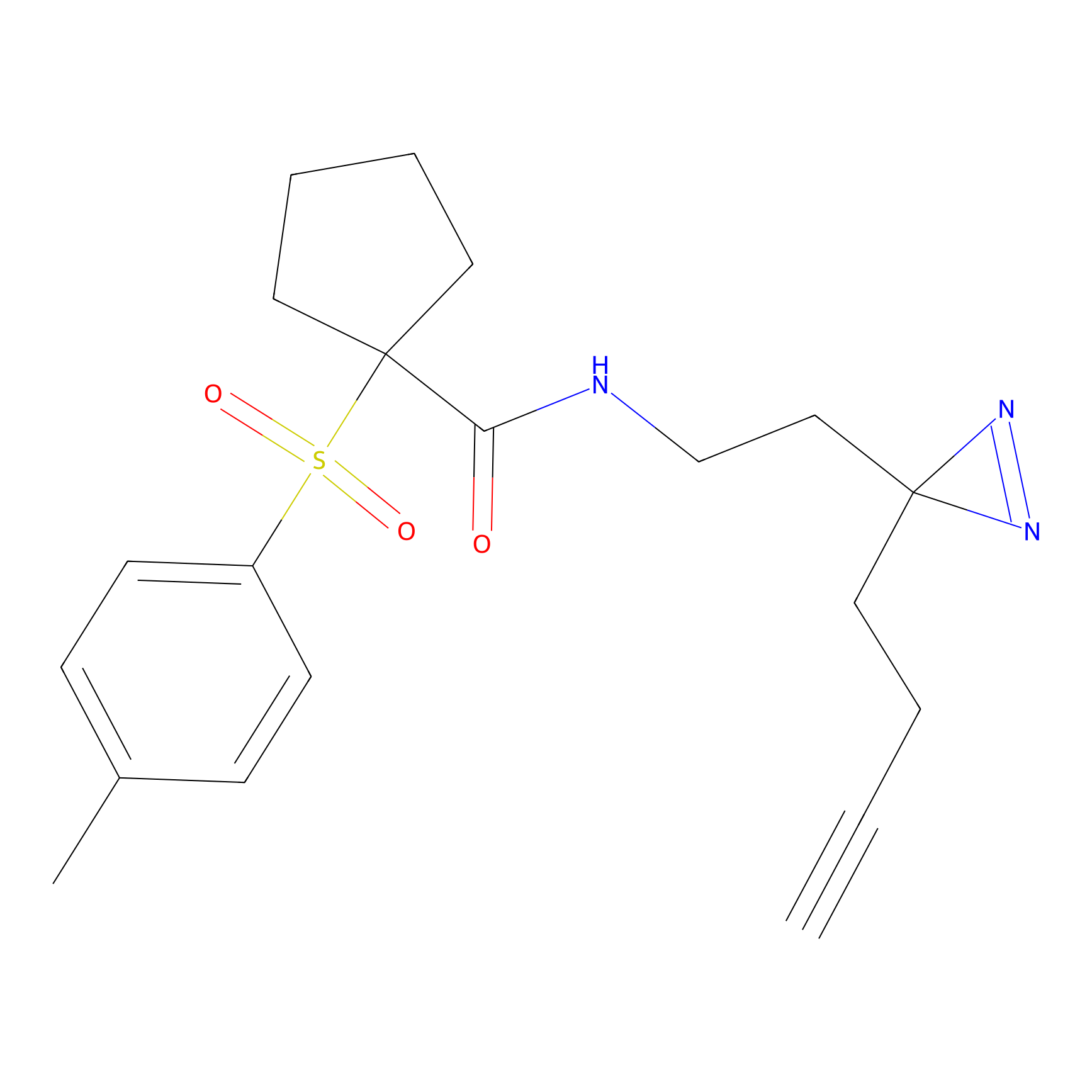
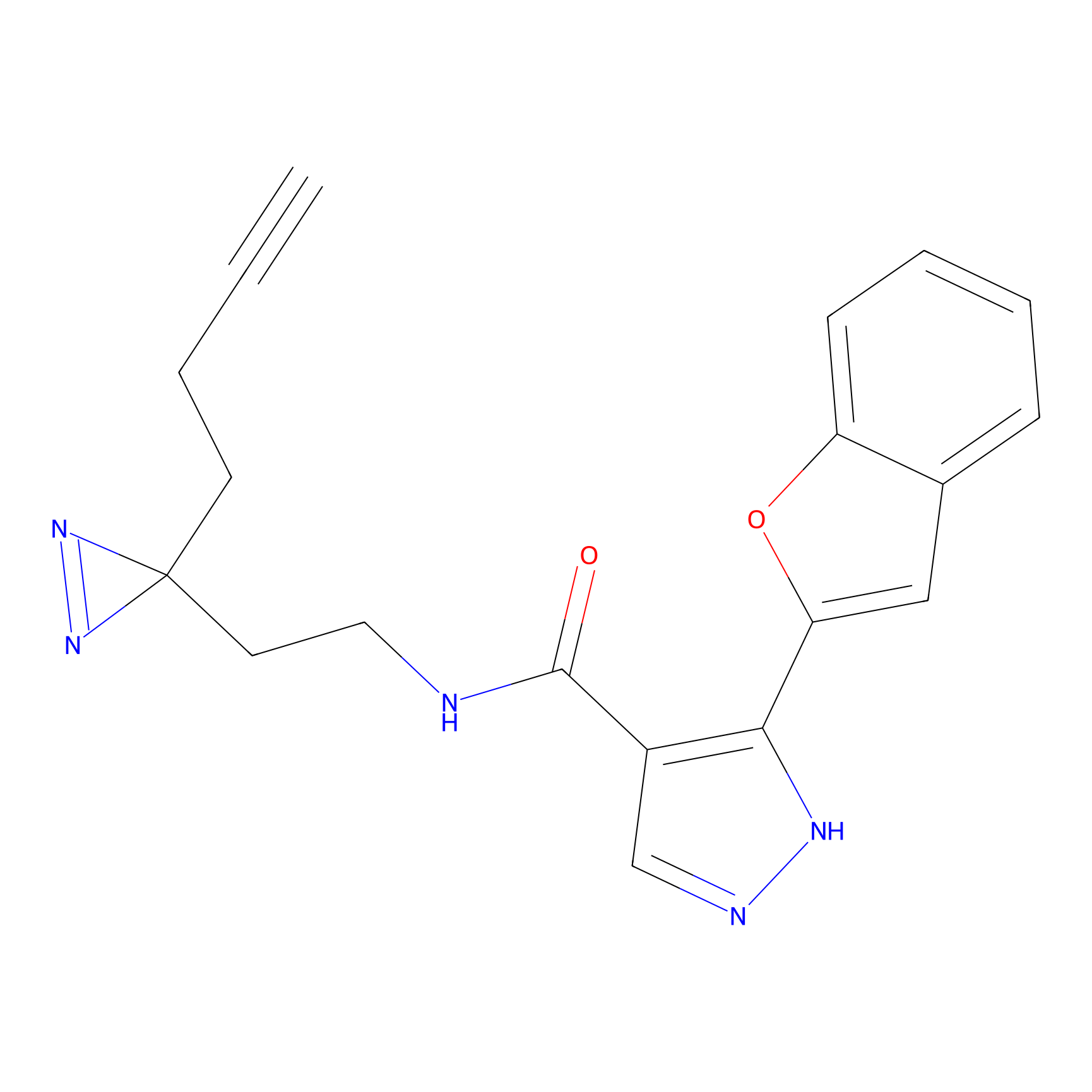
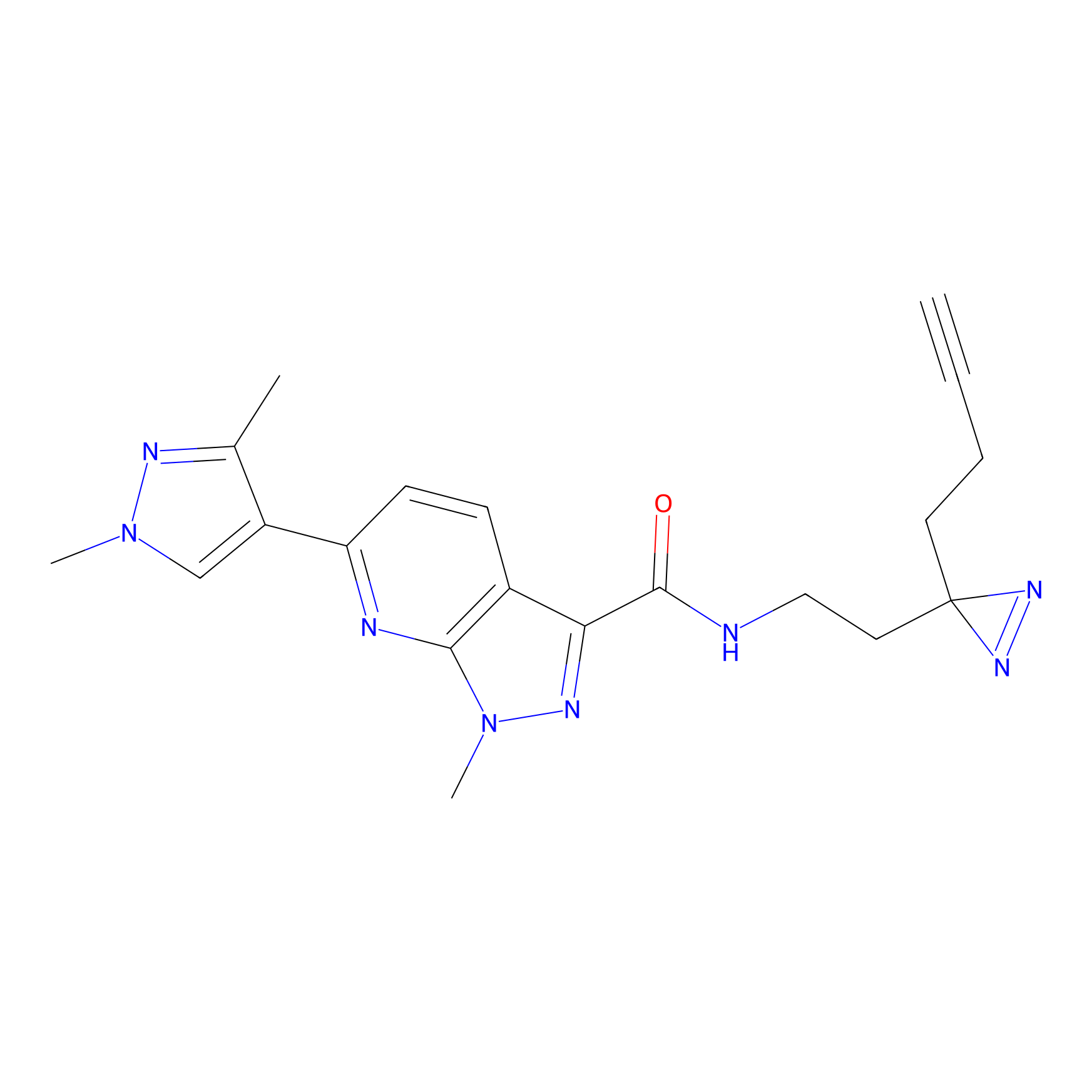
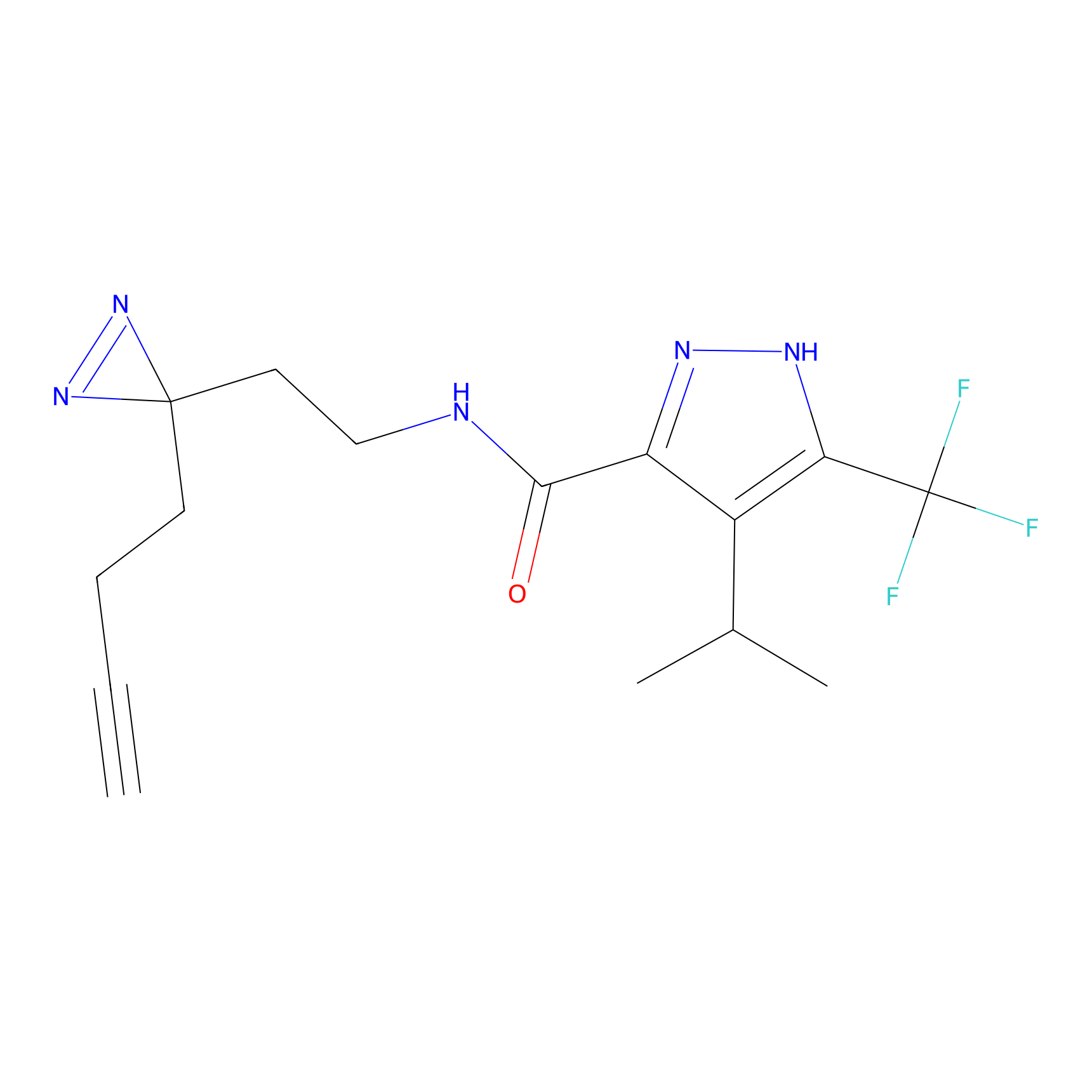
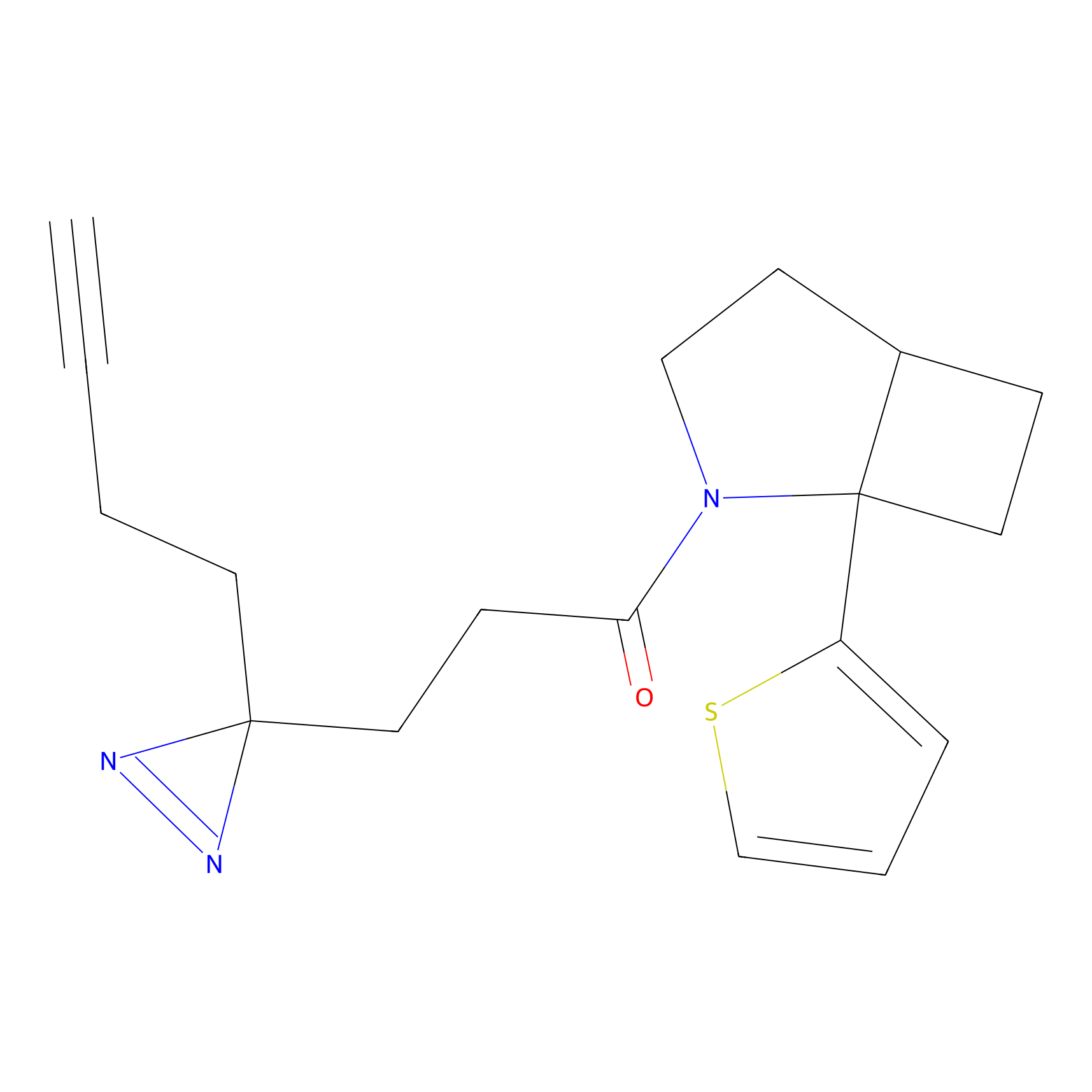
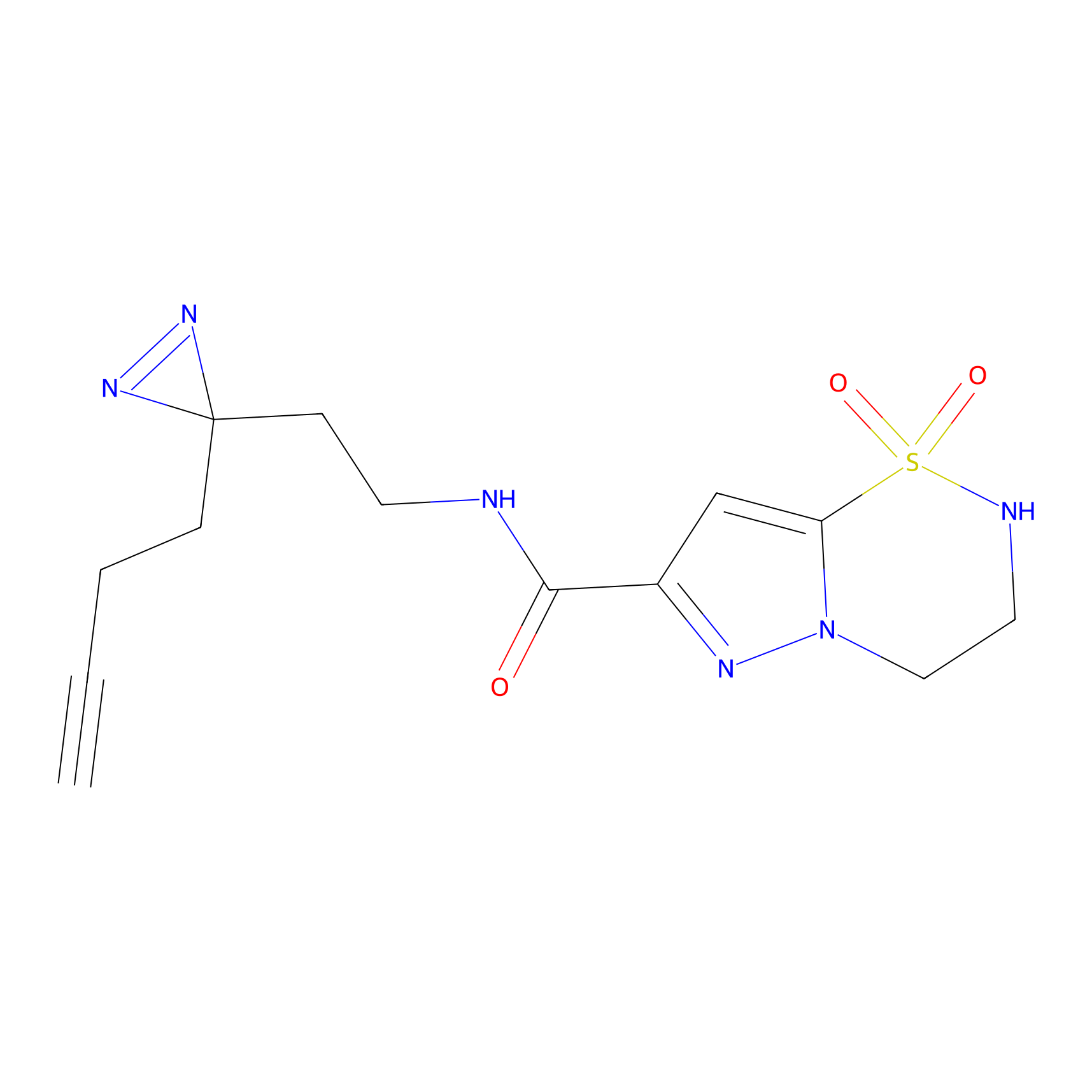
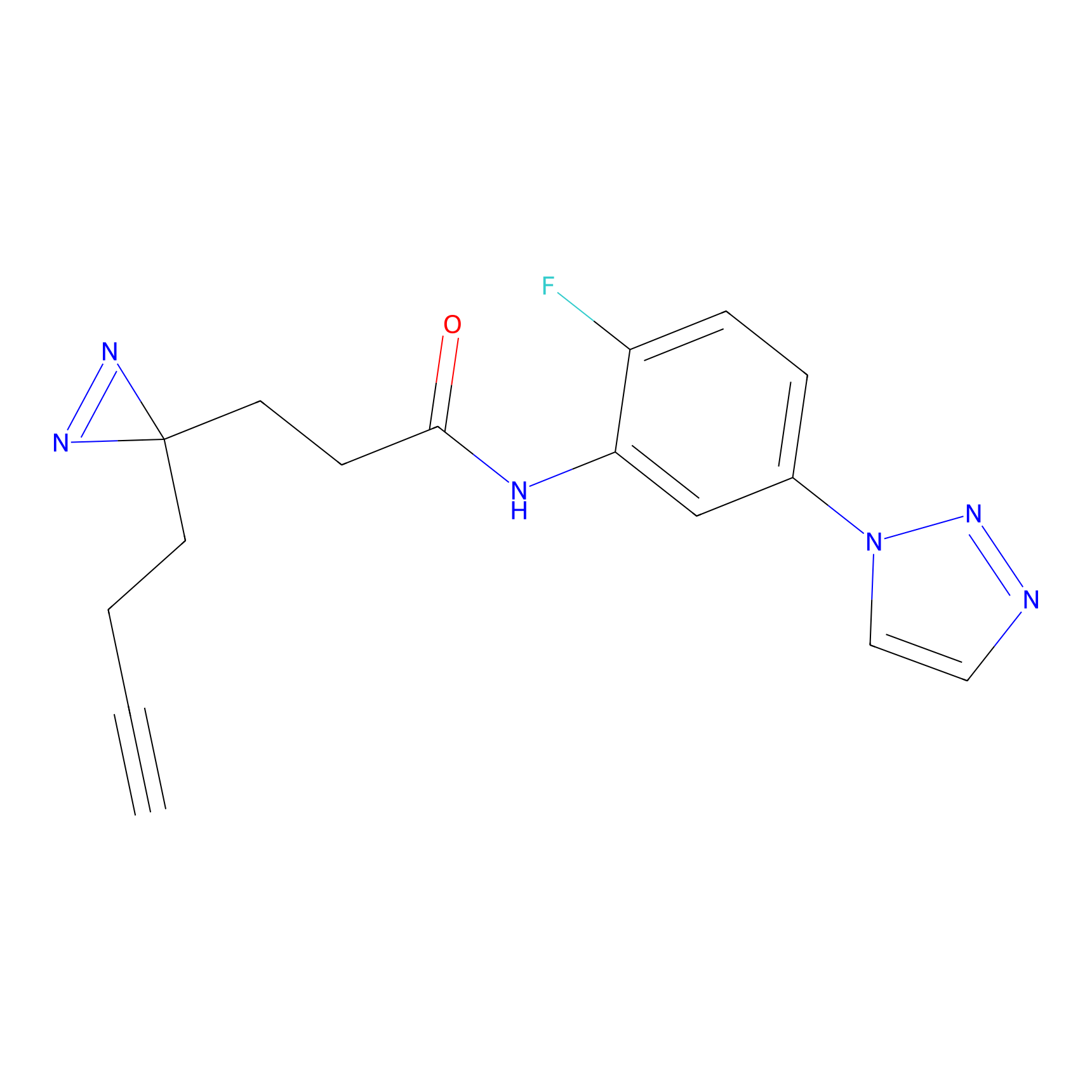
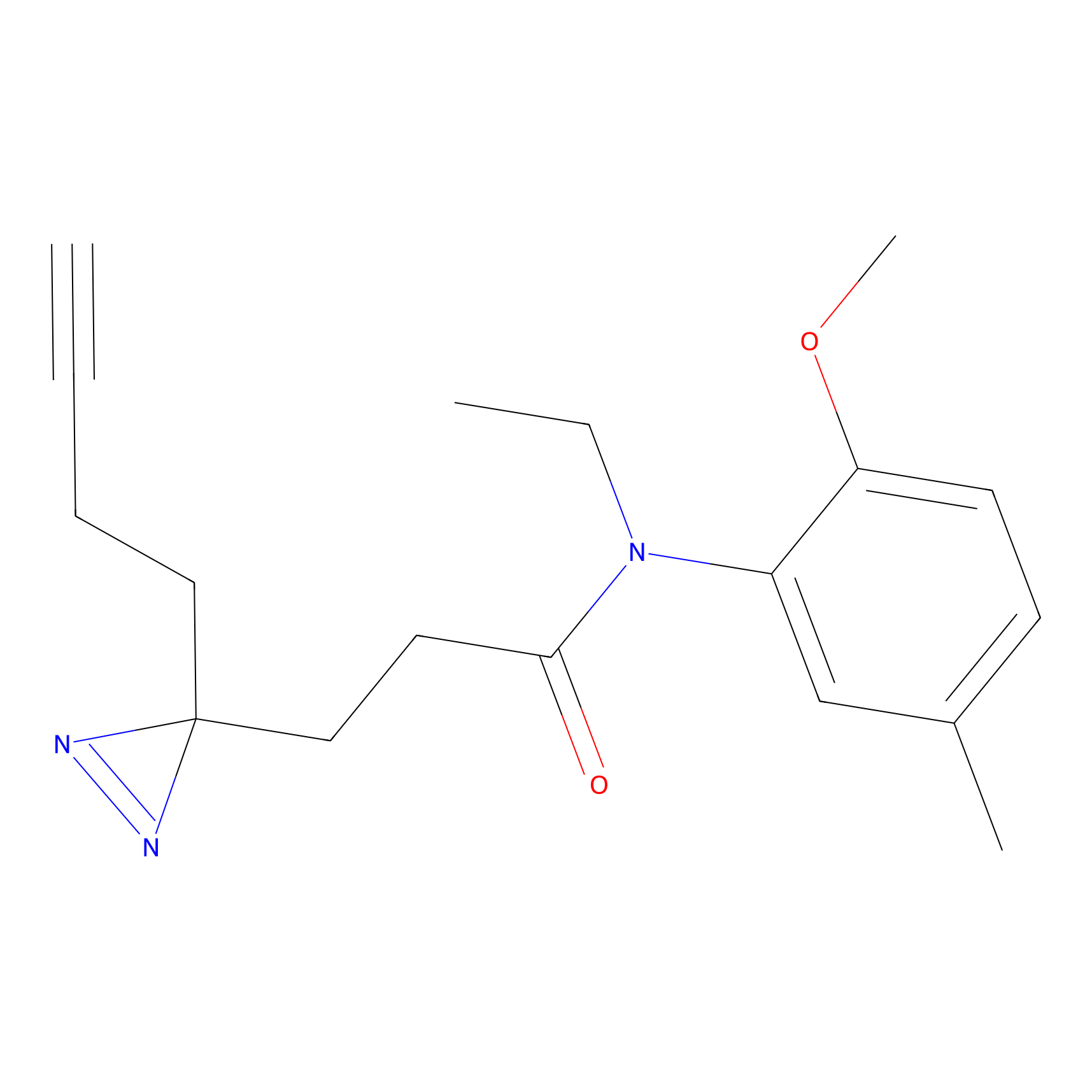
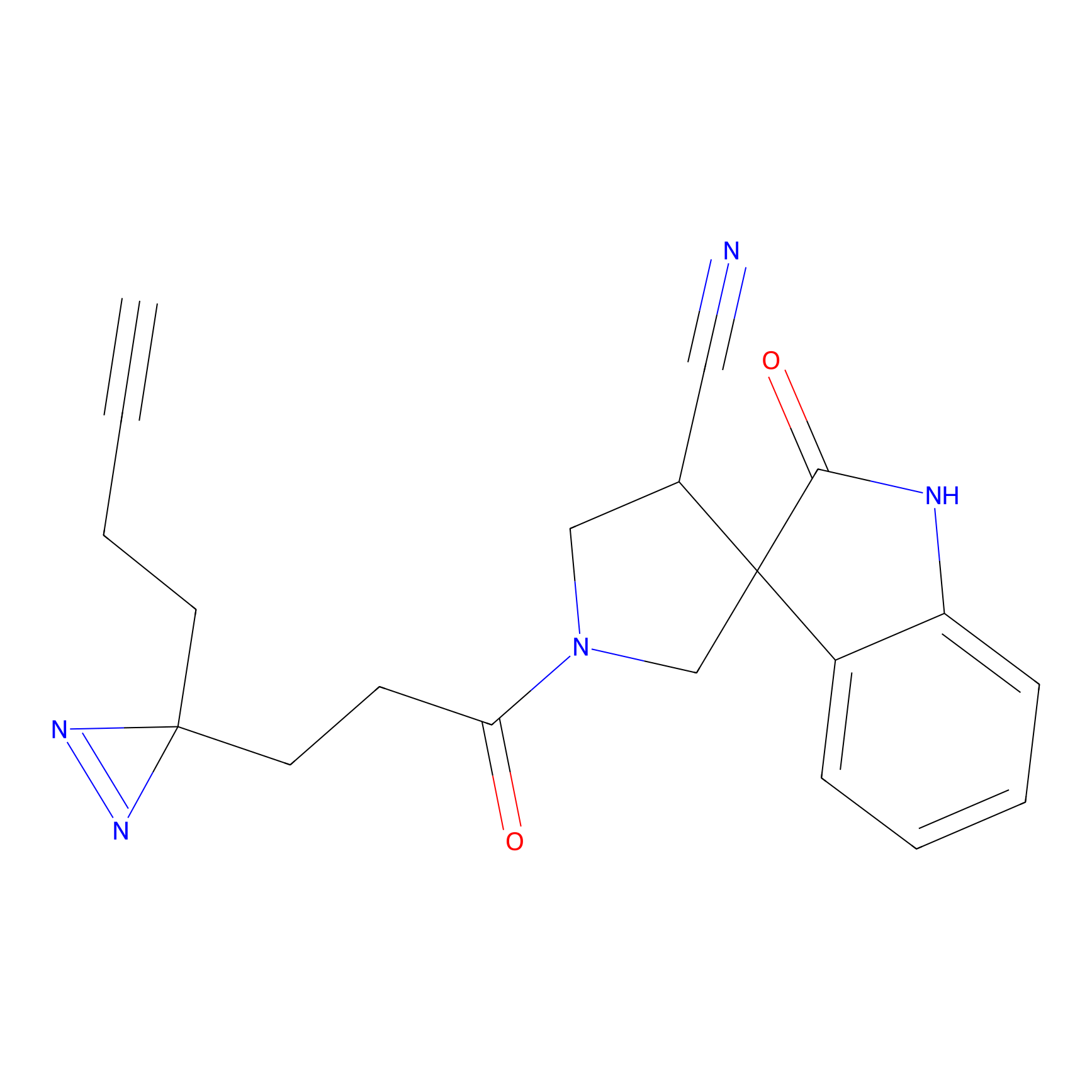
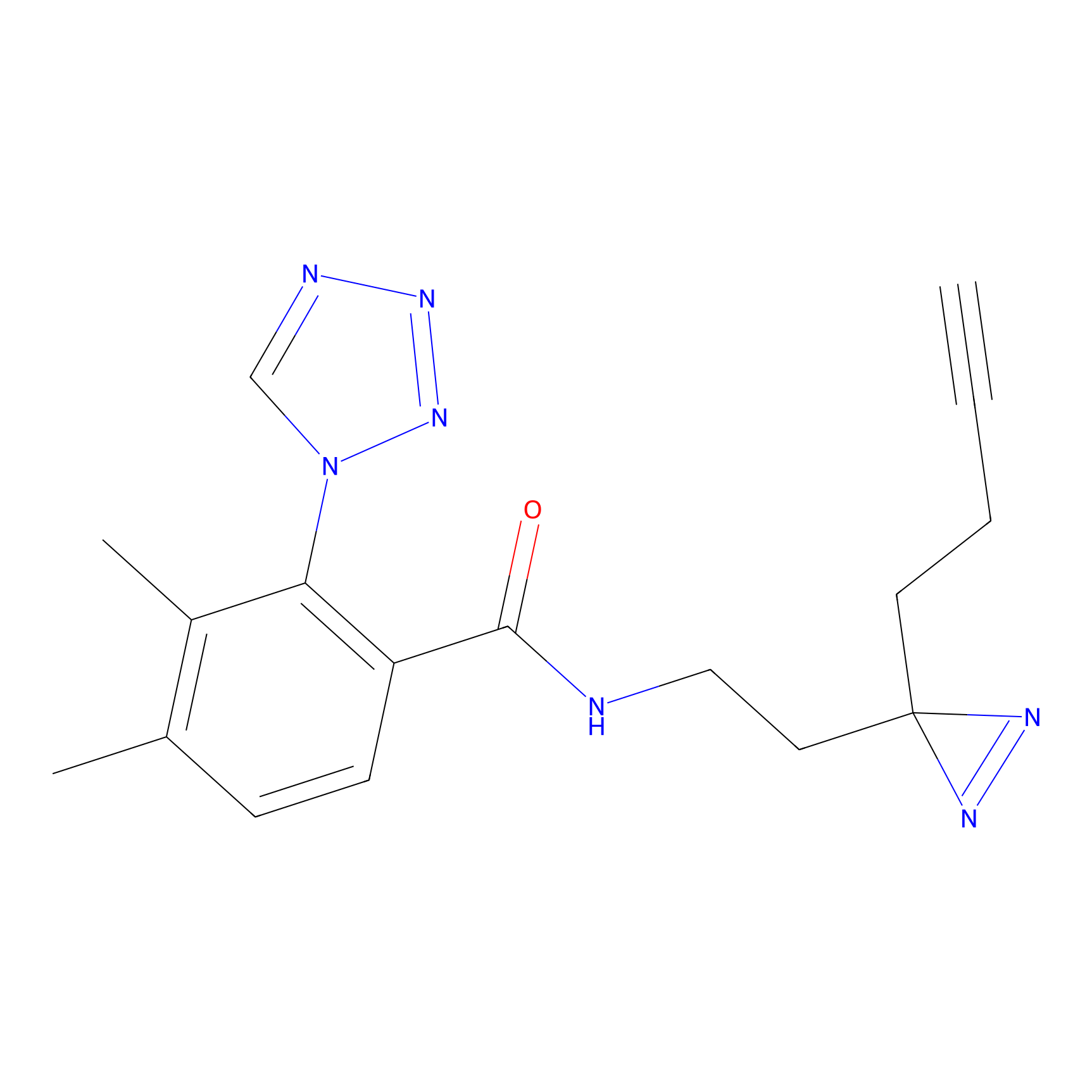
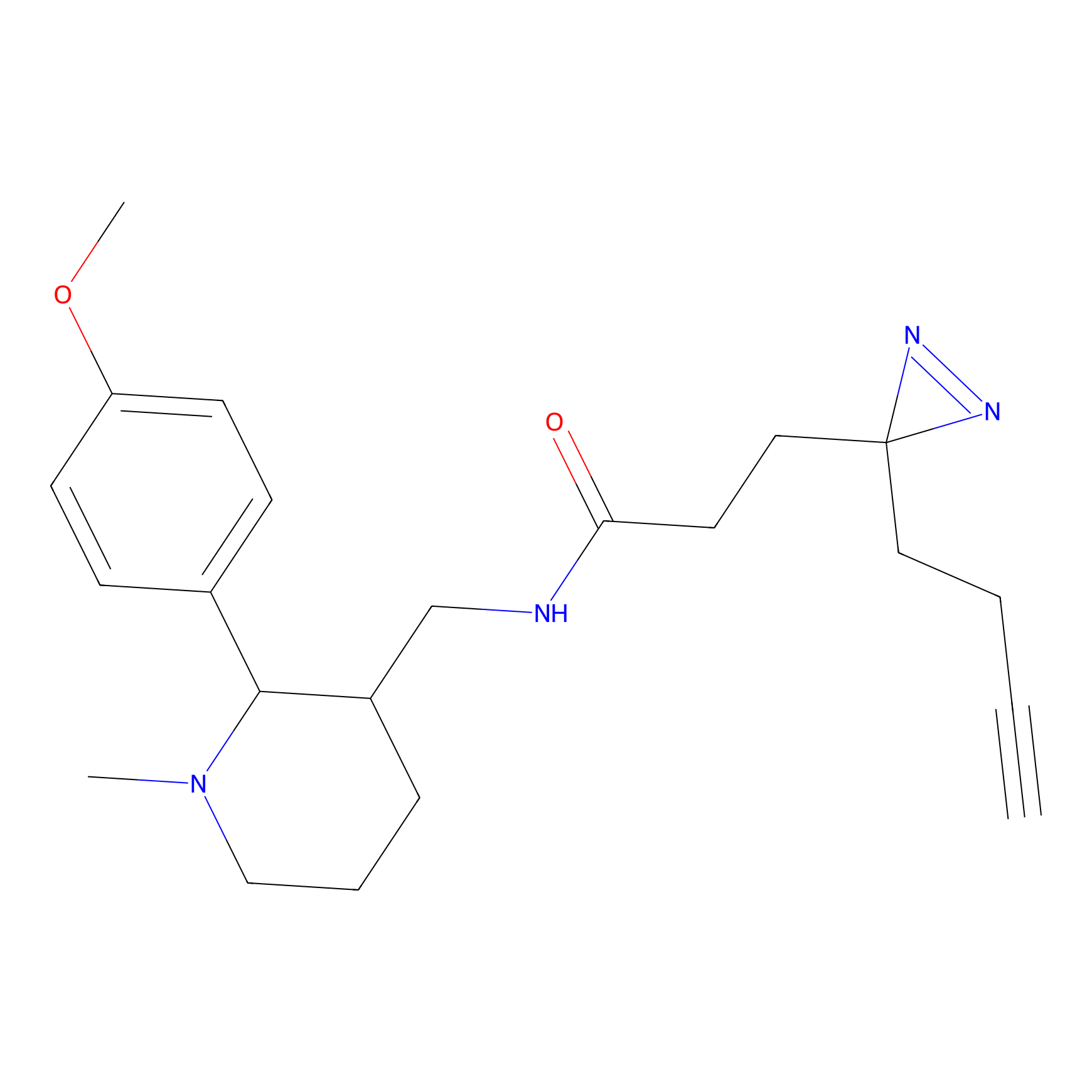
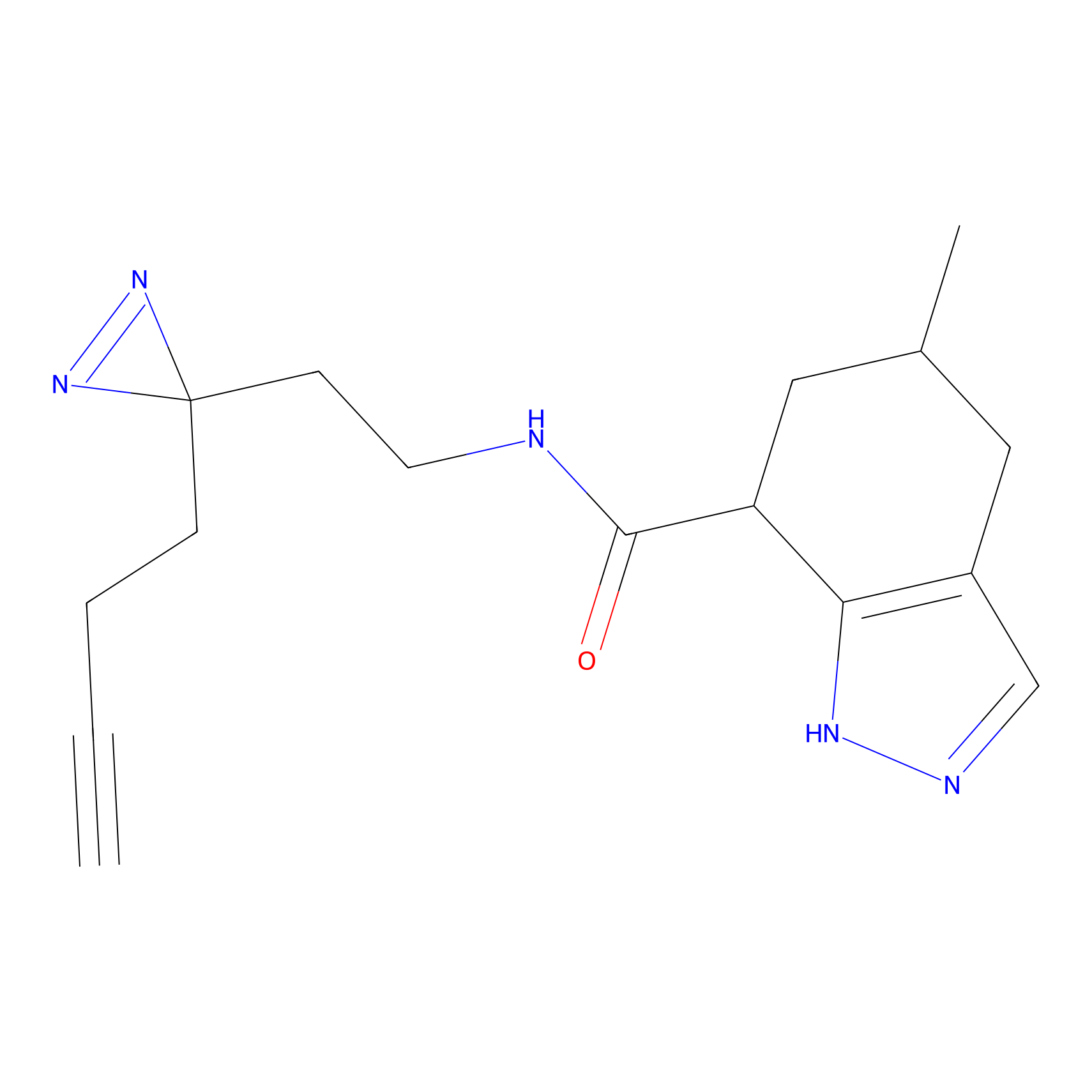
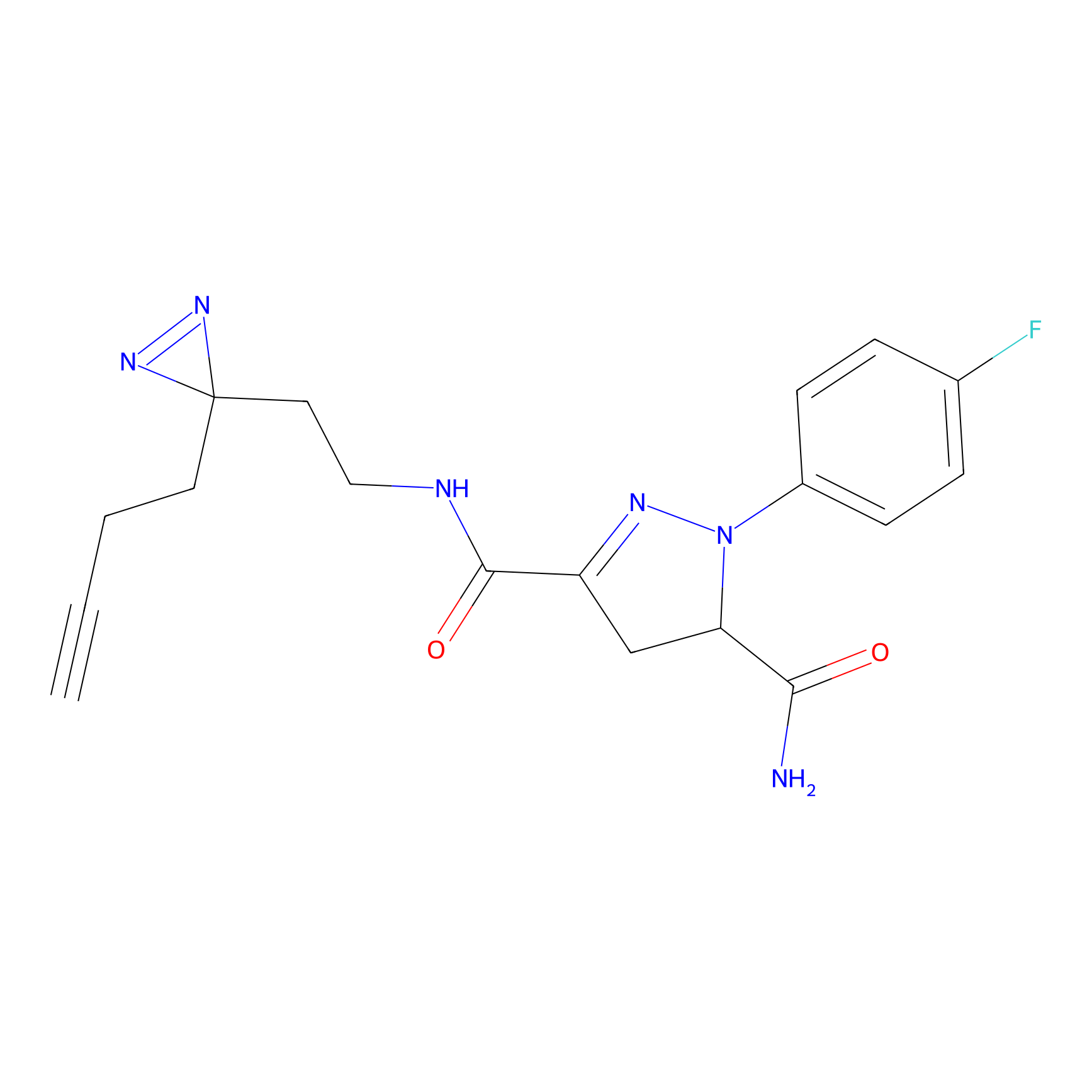
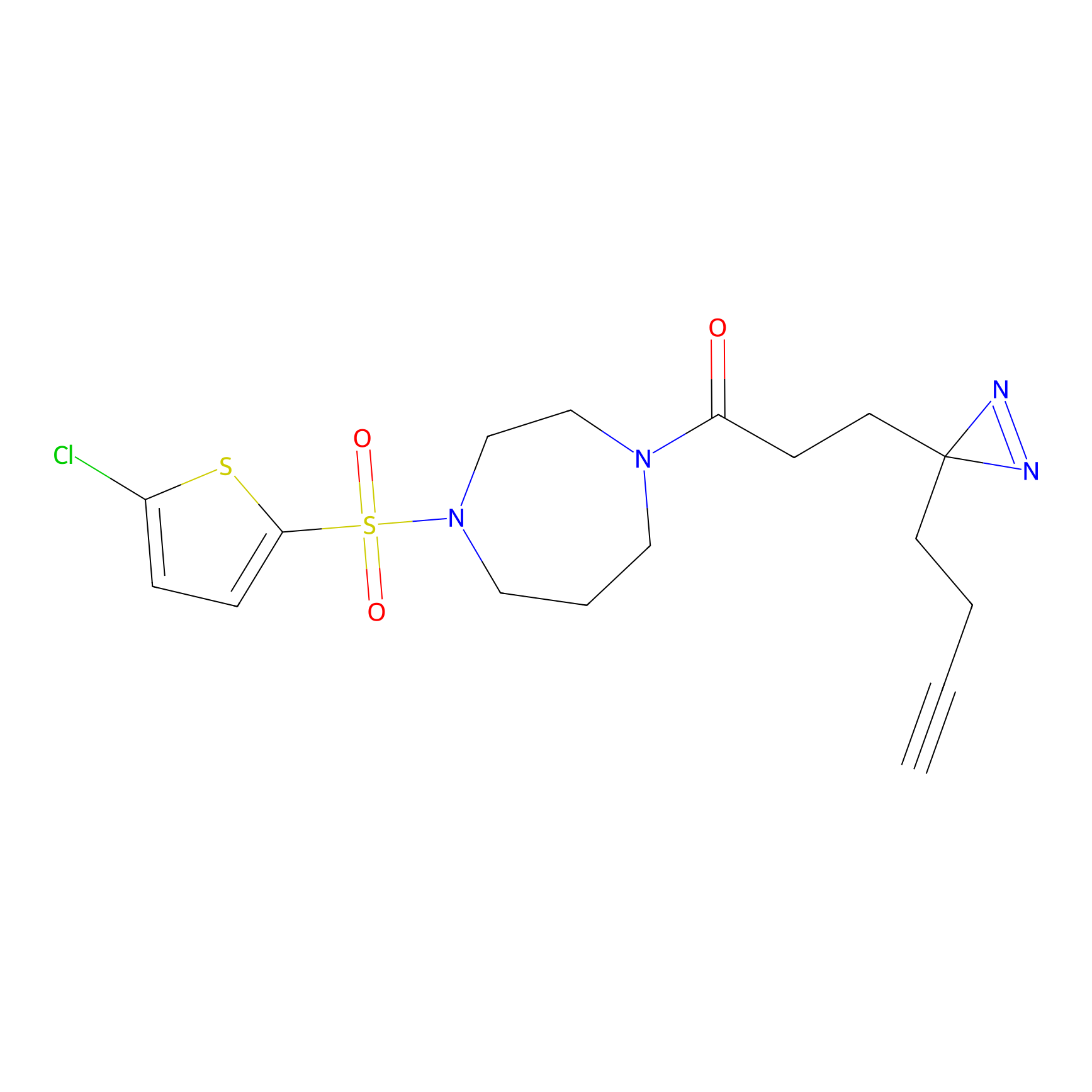
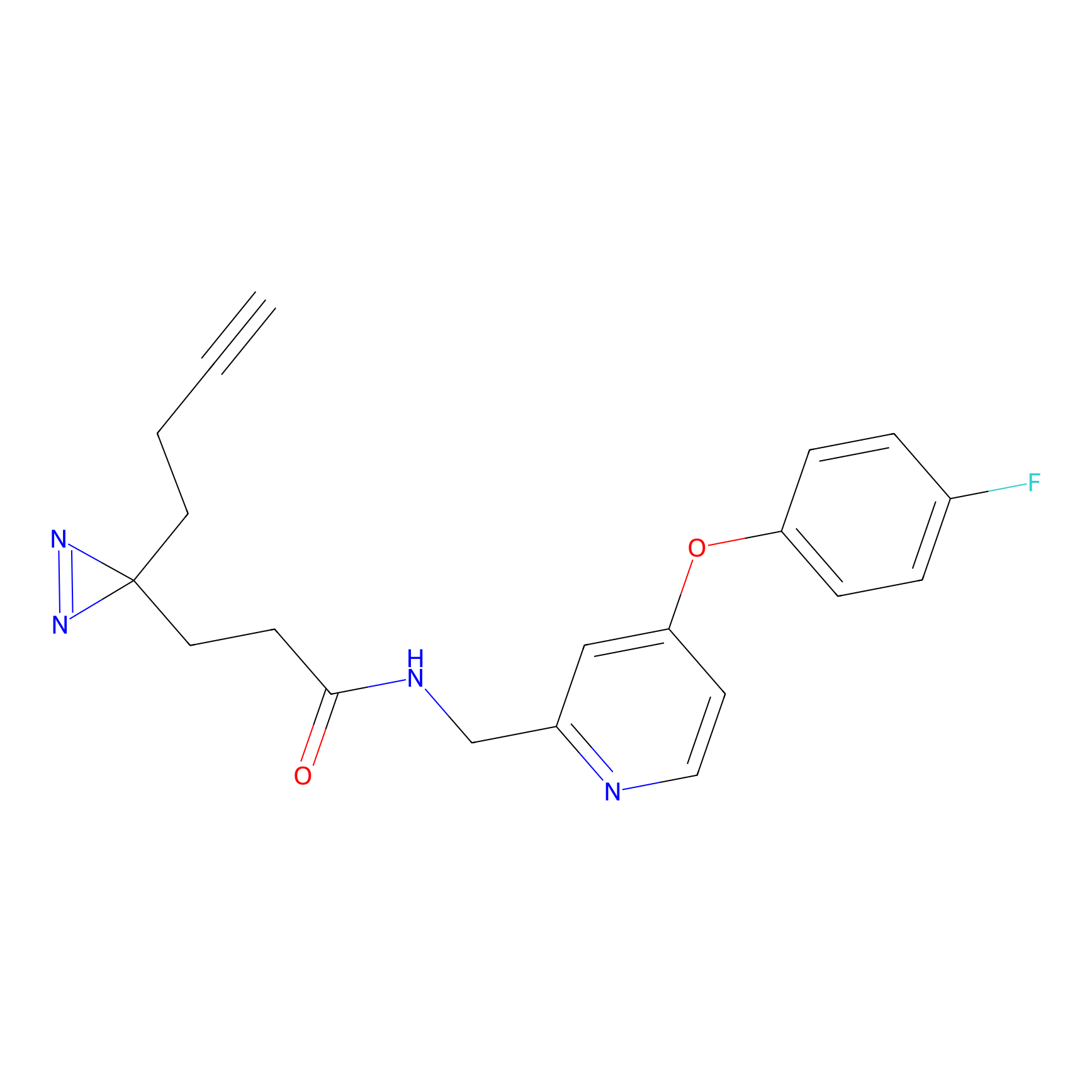
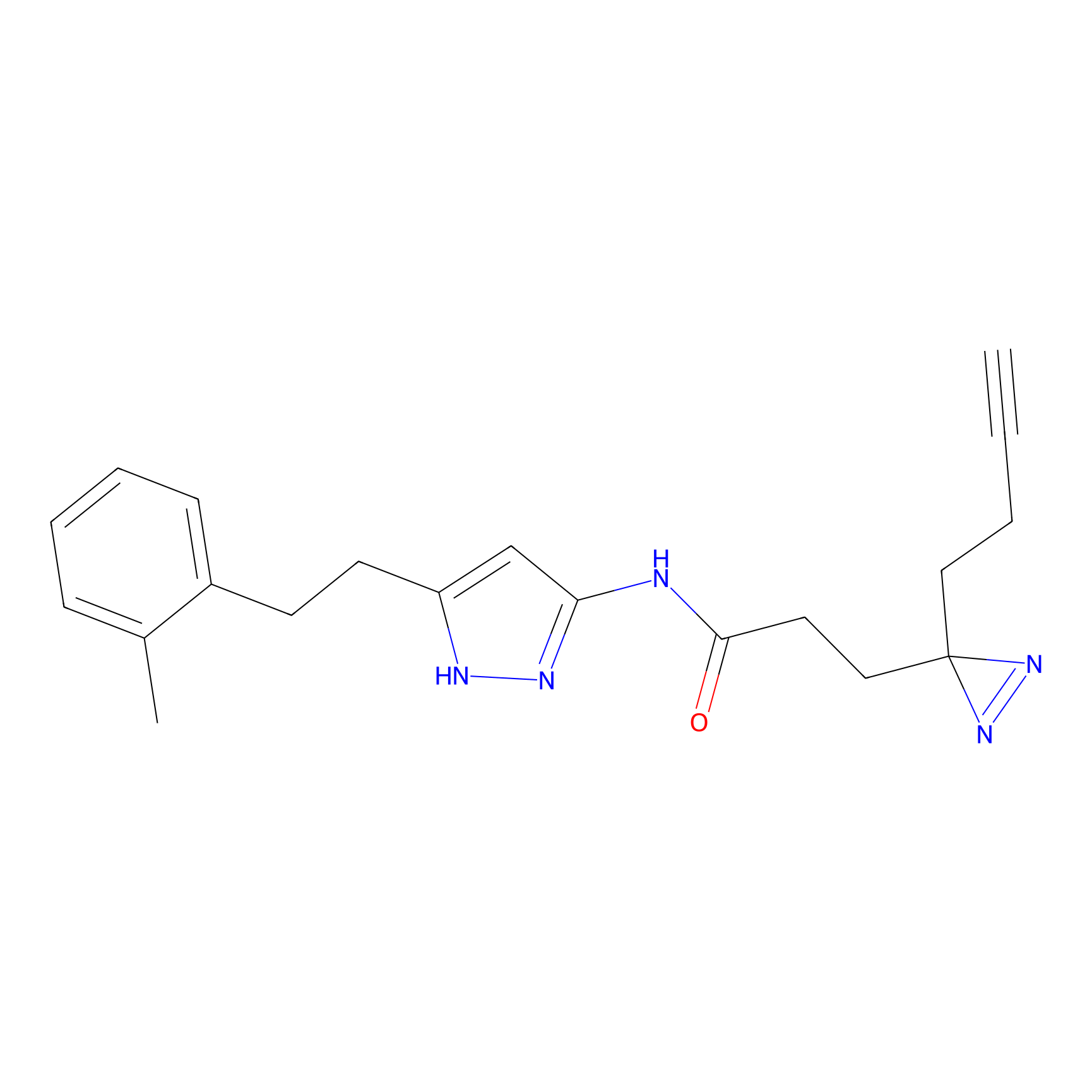
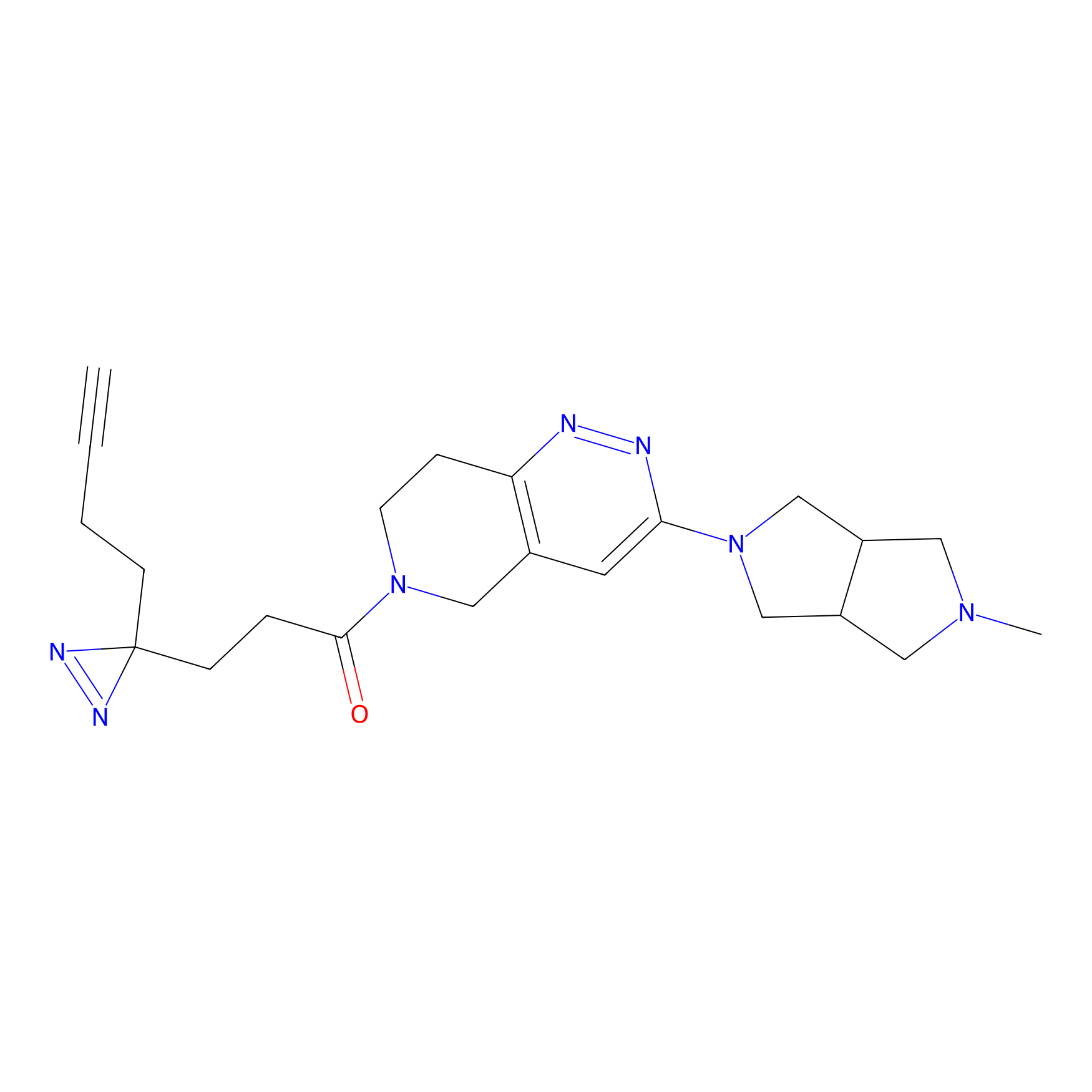
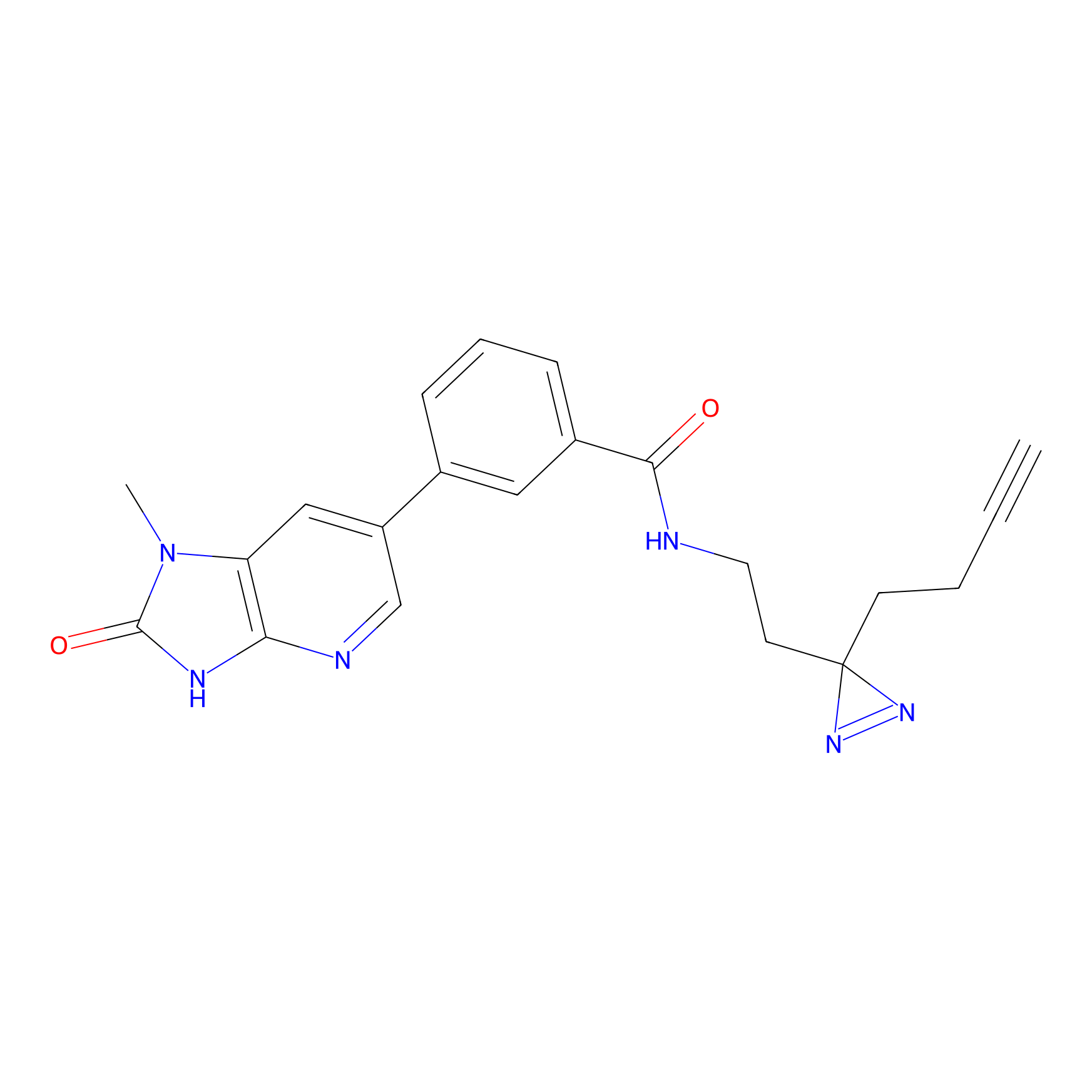
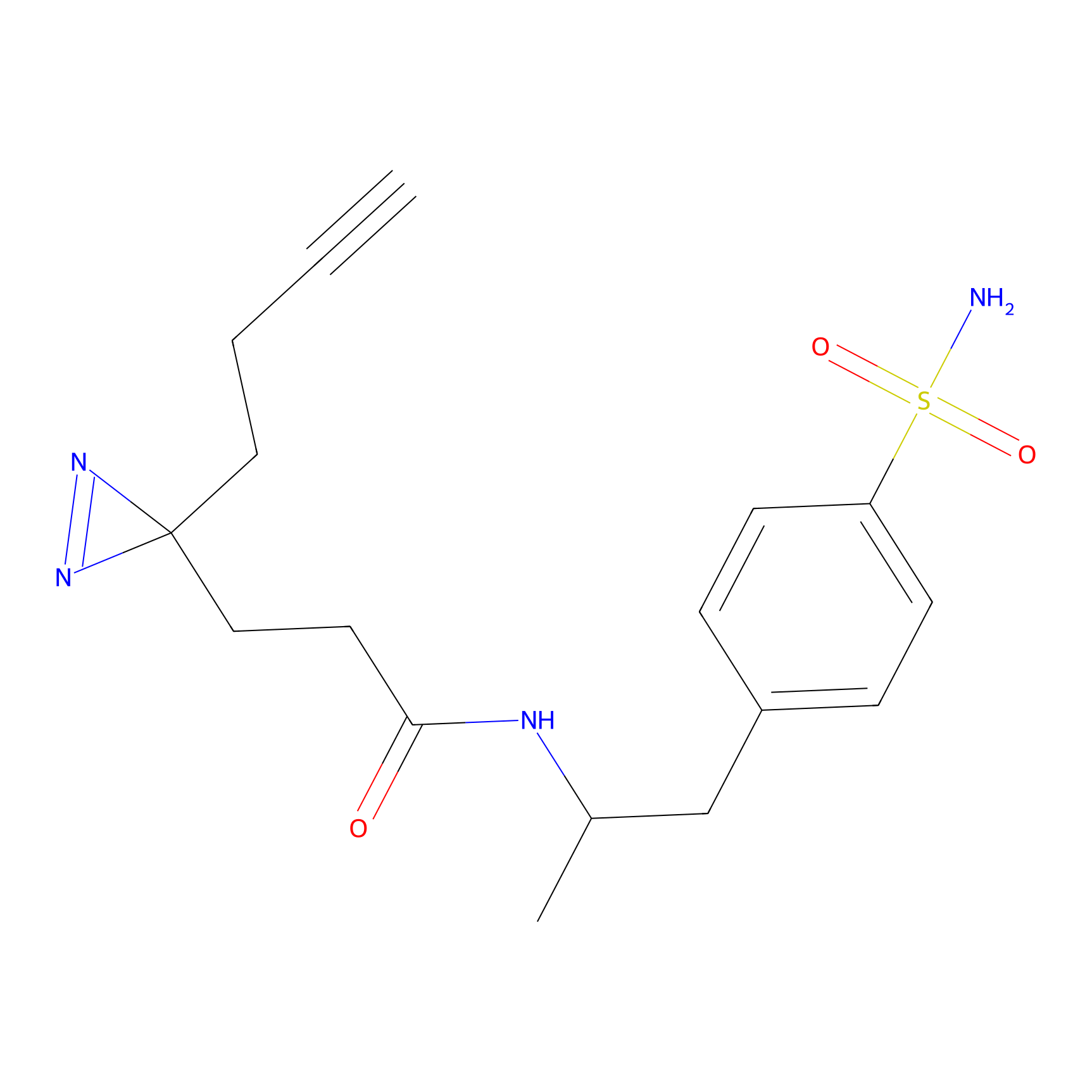
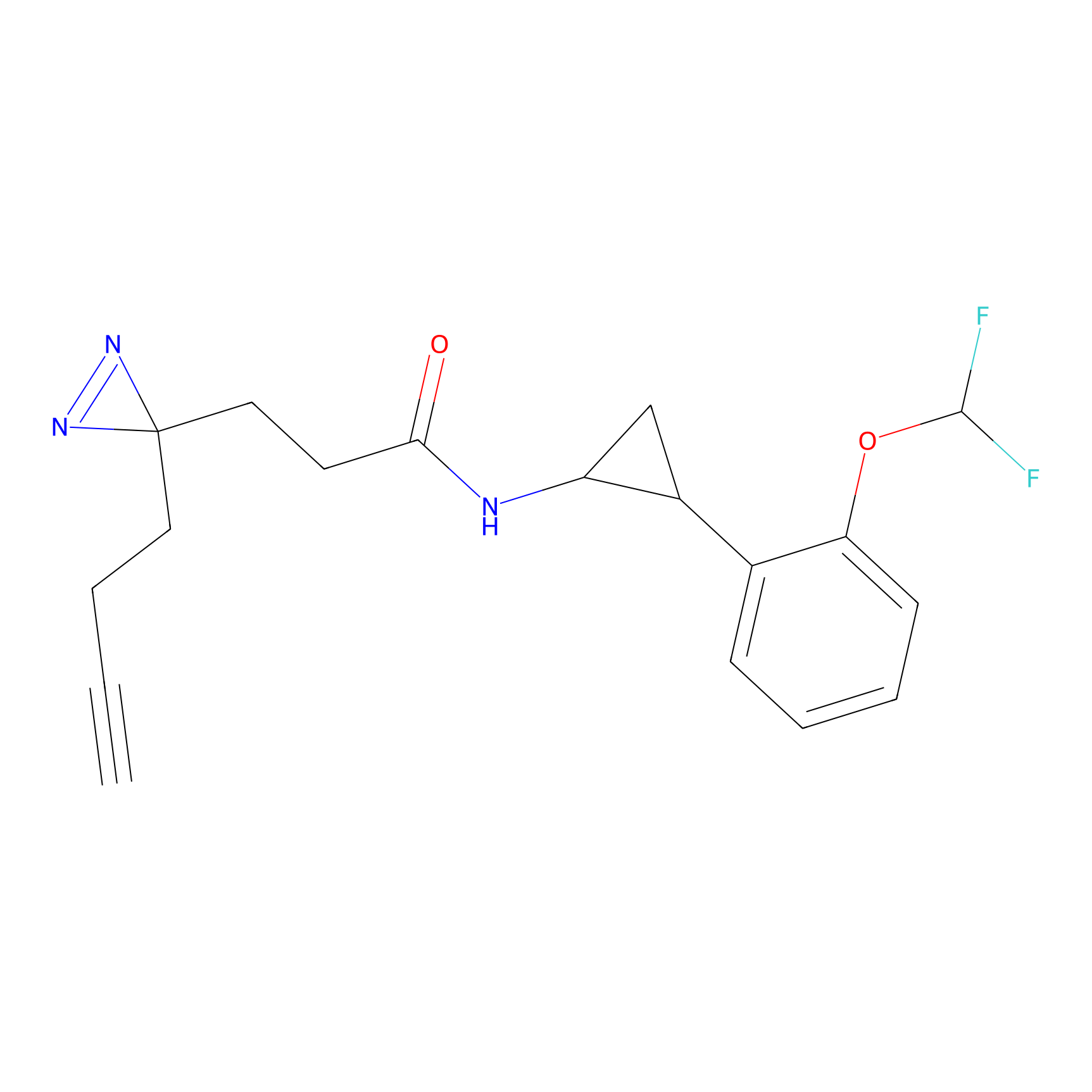
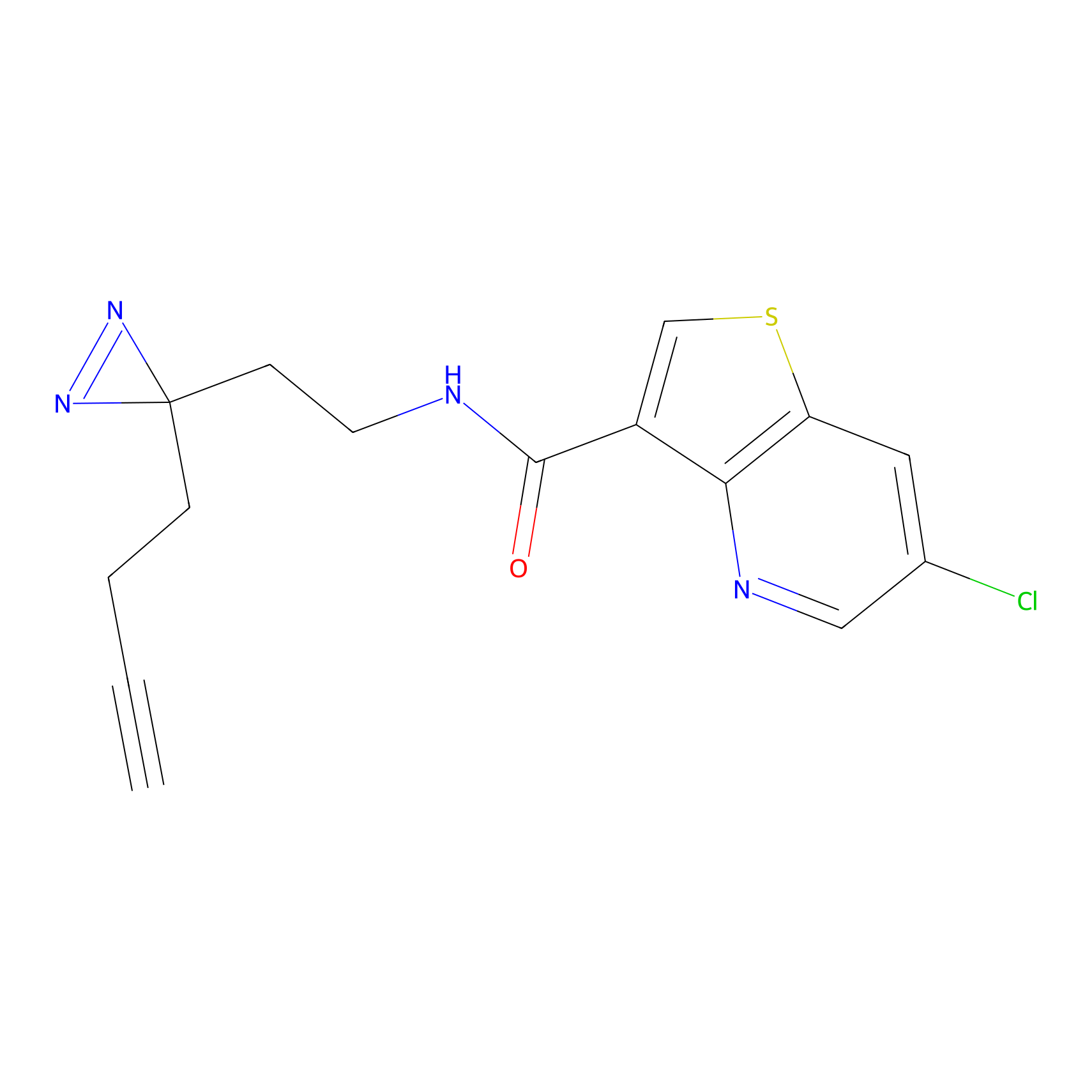
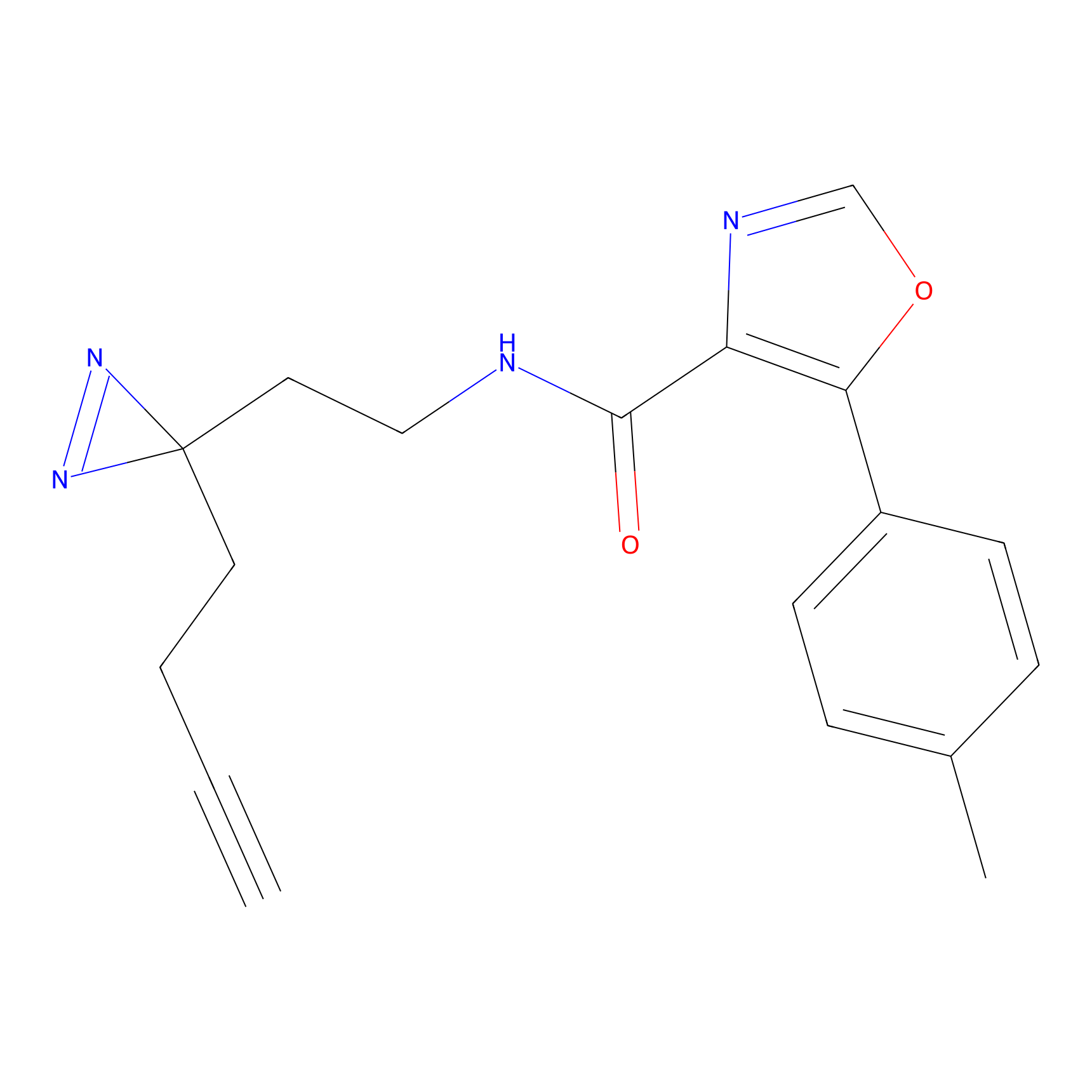
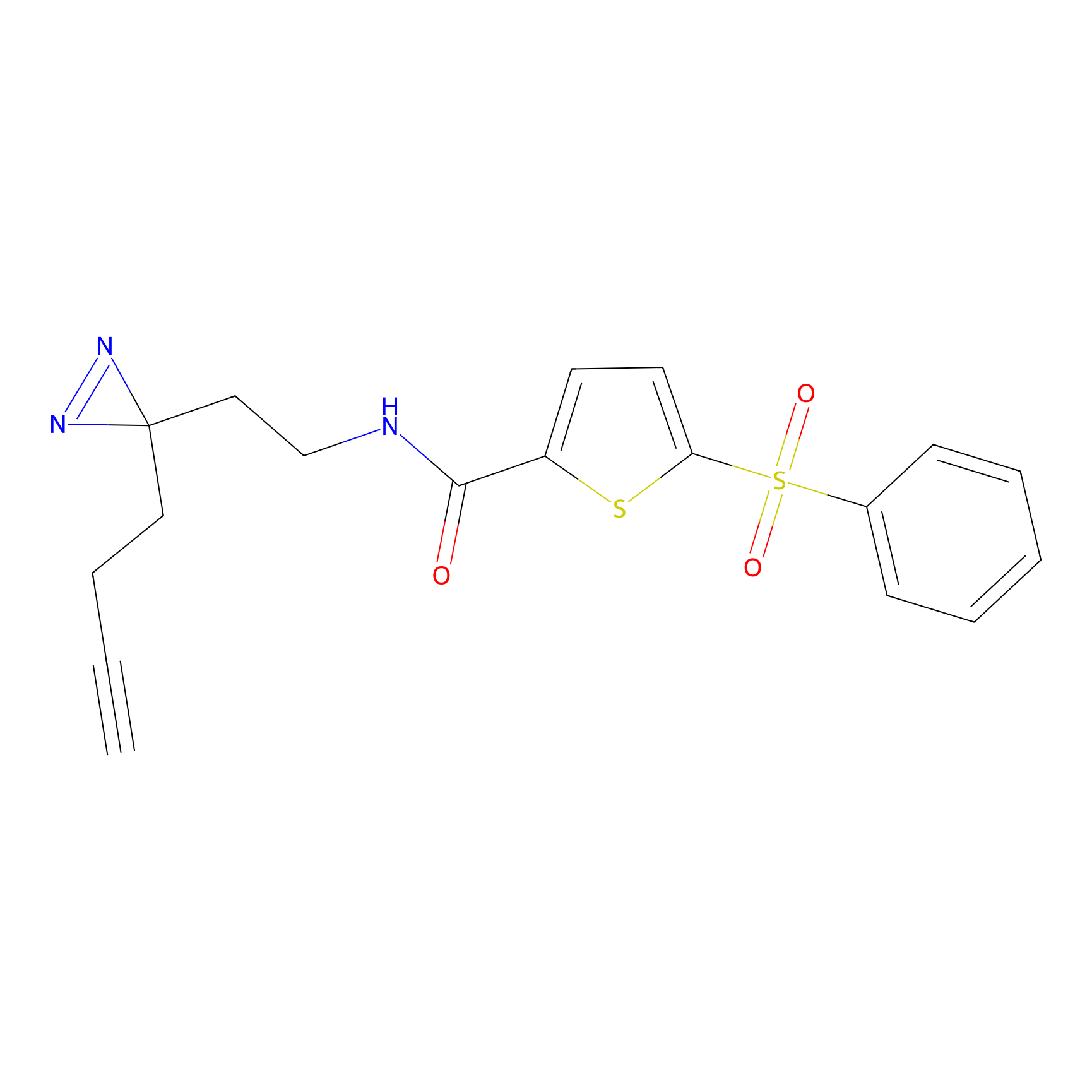
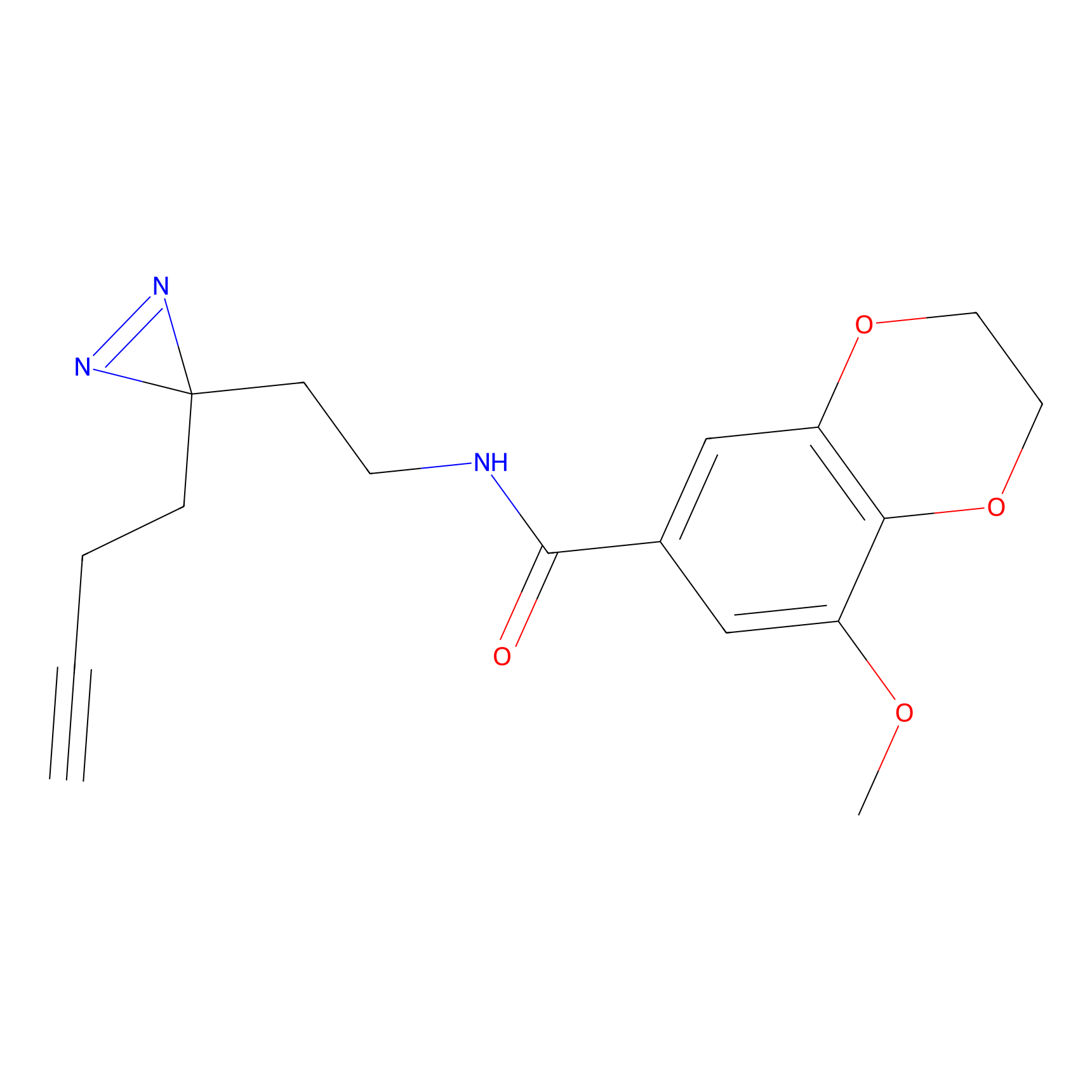
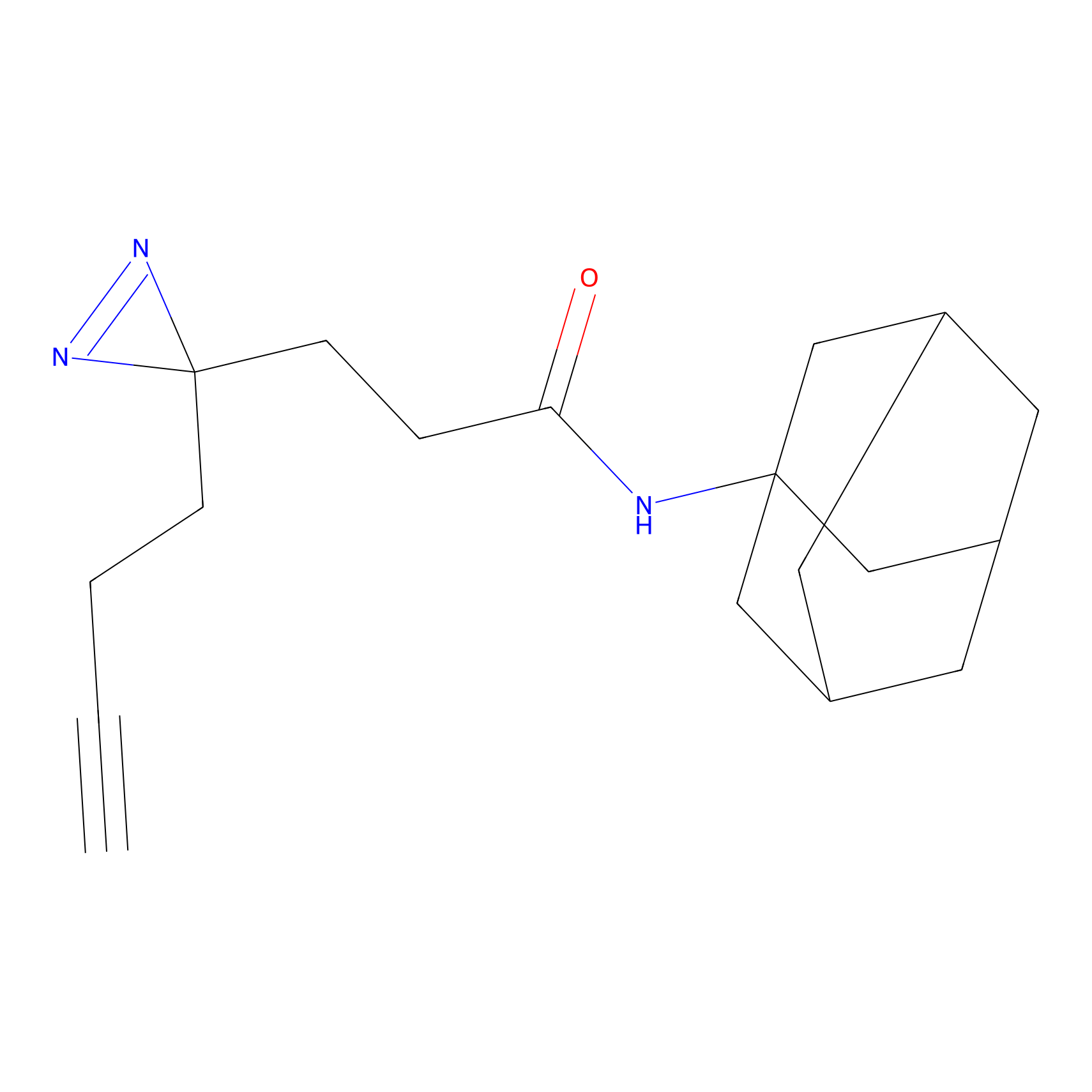
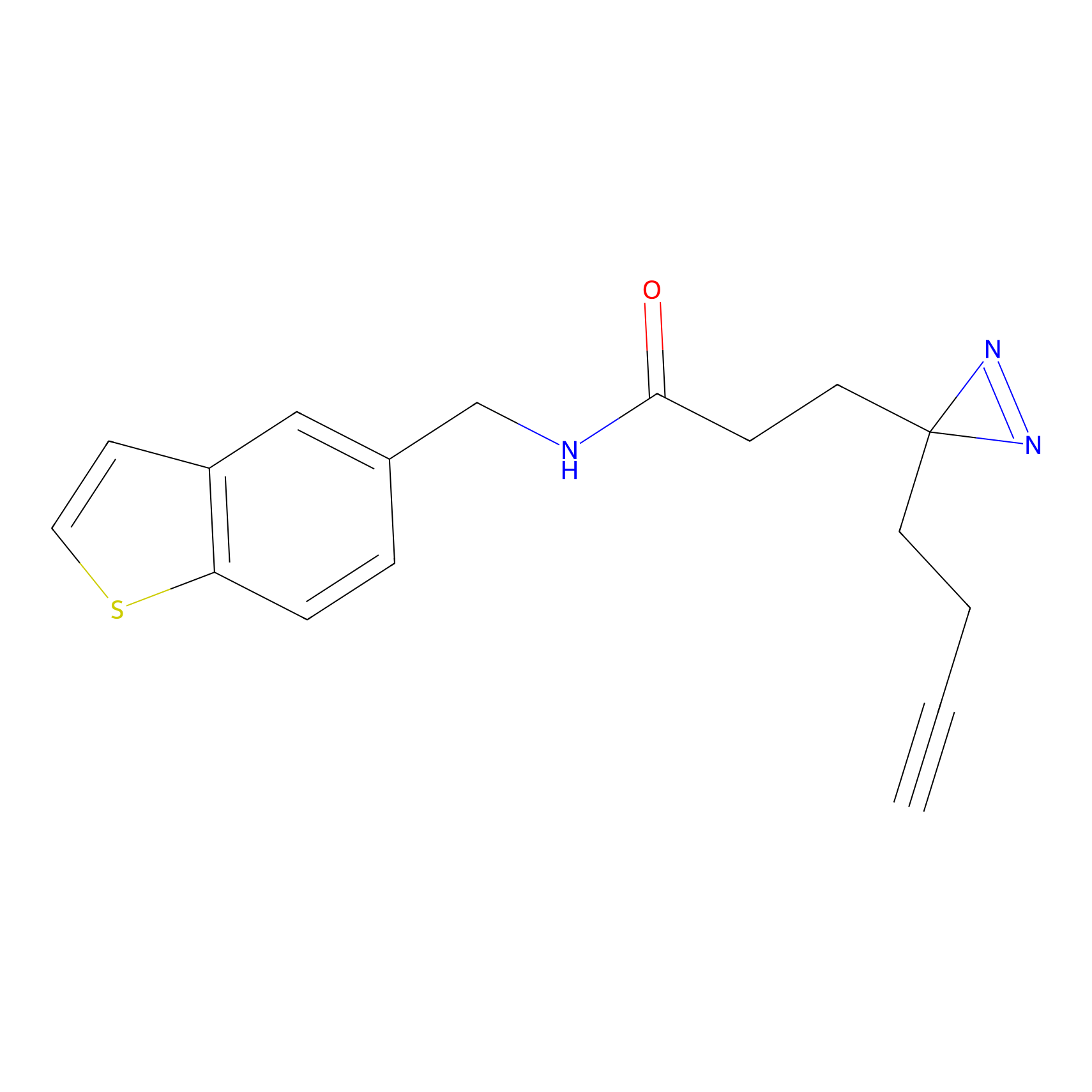
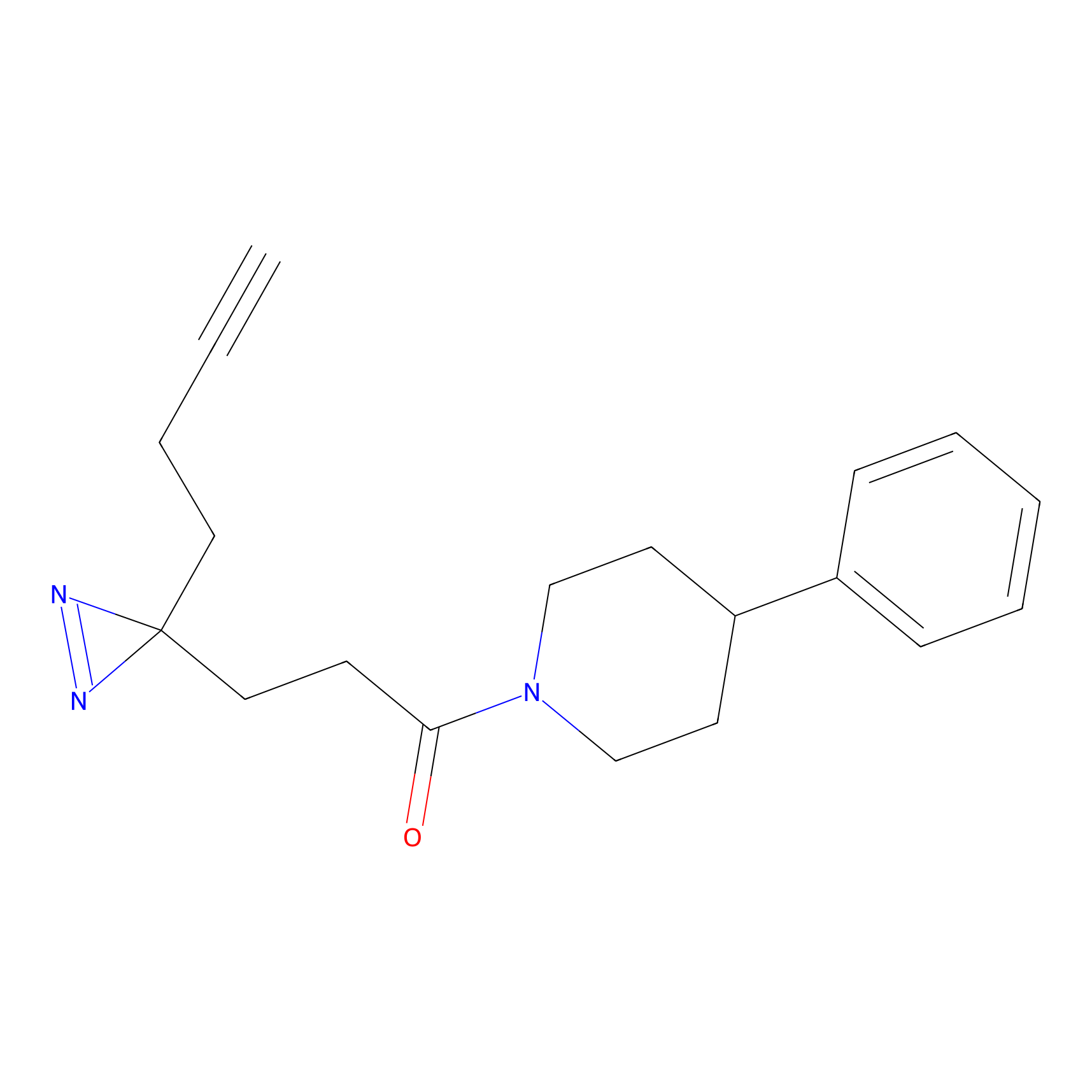
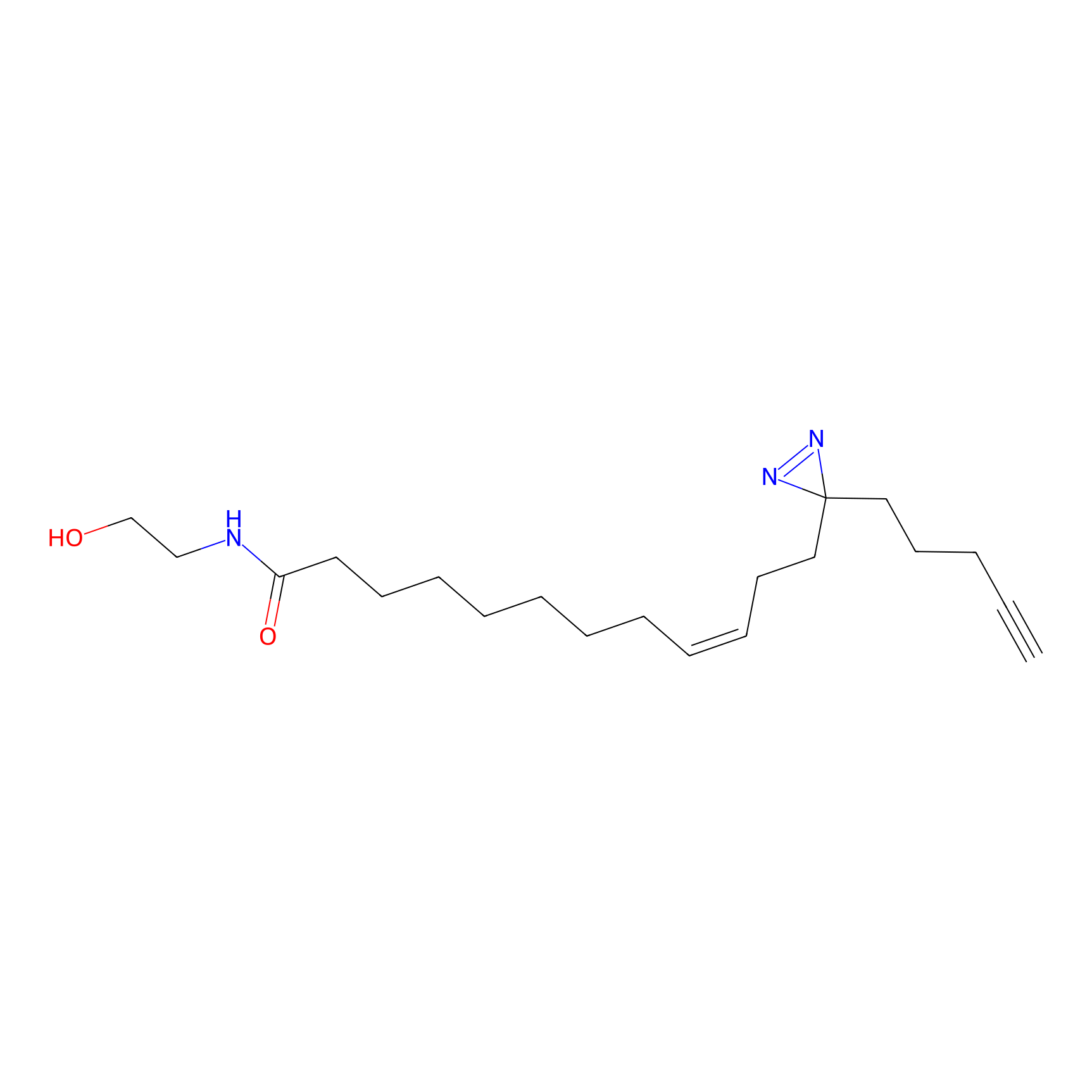
TH216 Probe Info |
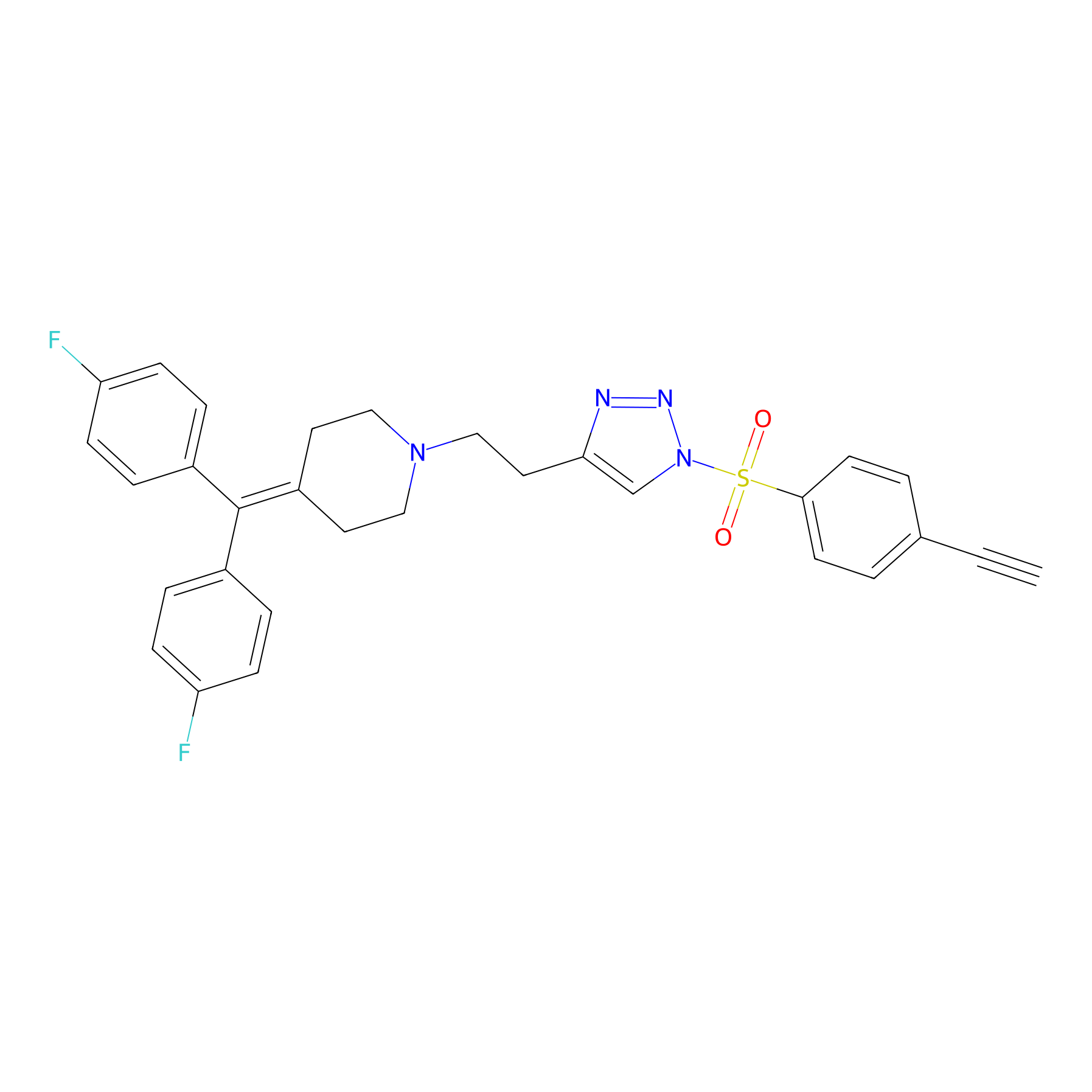 |
Y97(20.00) | LDD0259 | [2] | |
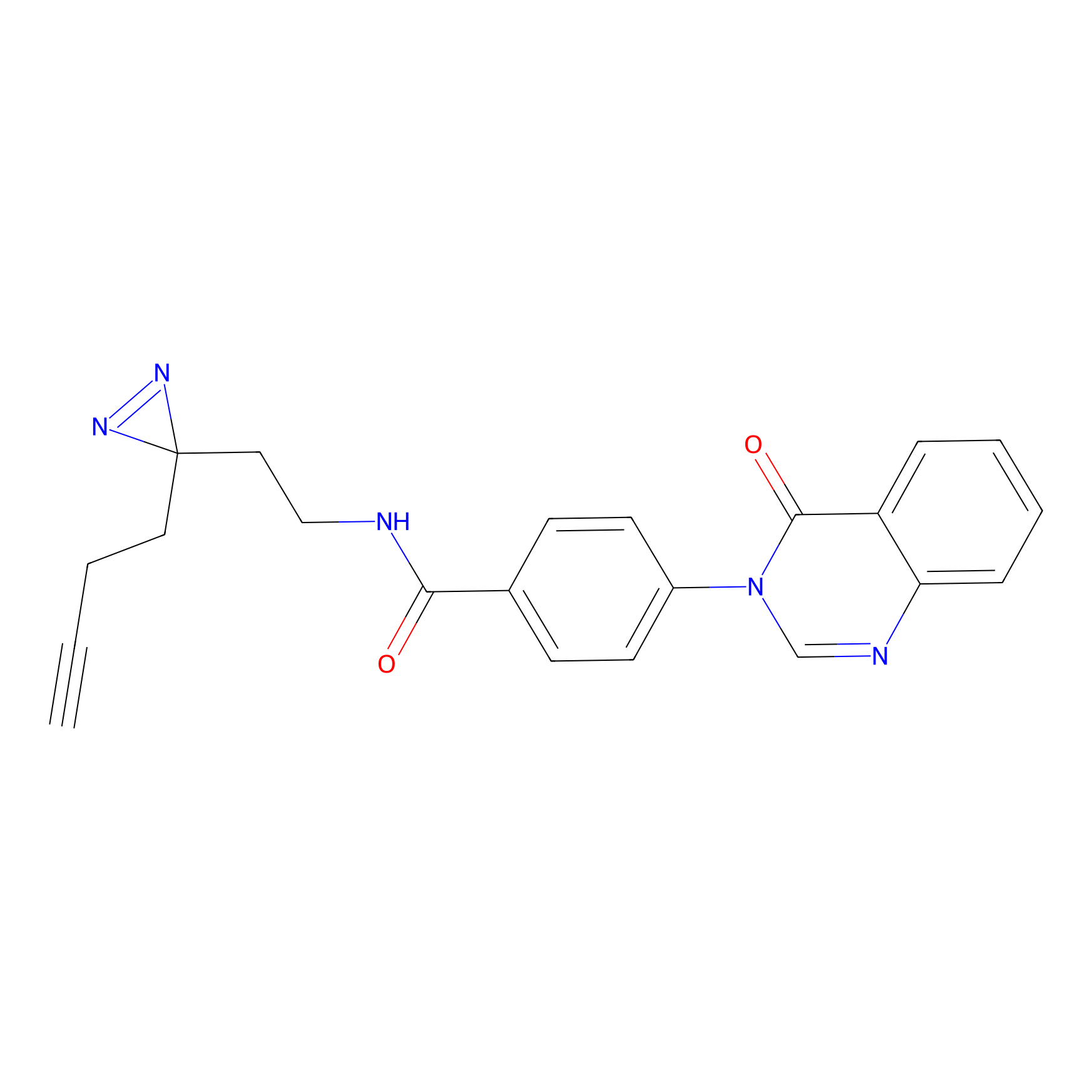
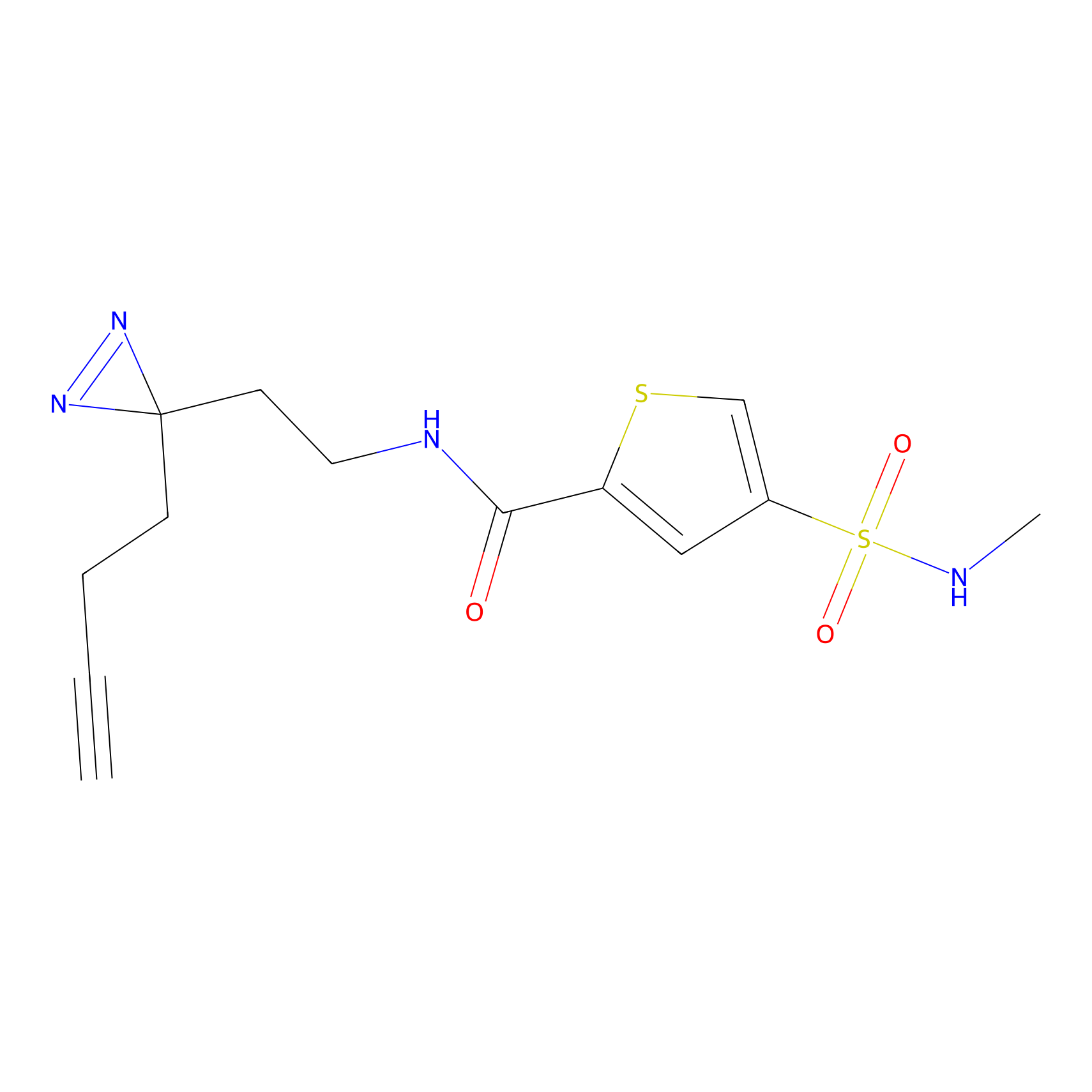
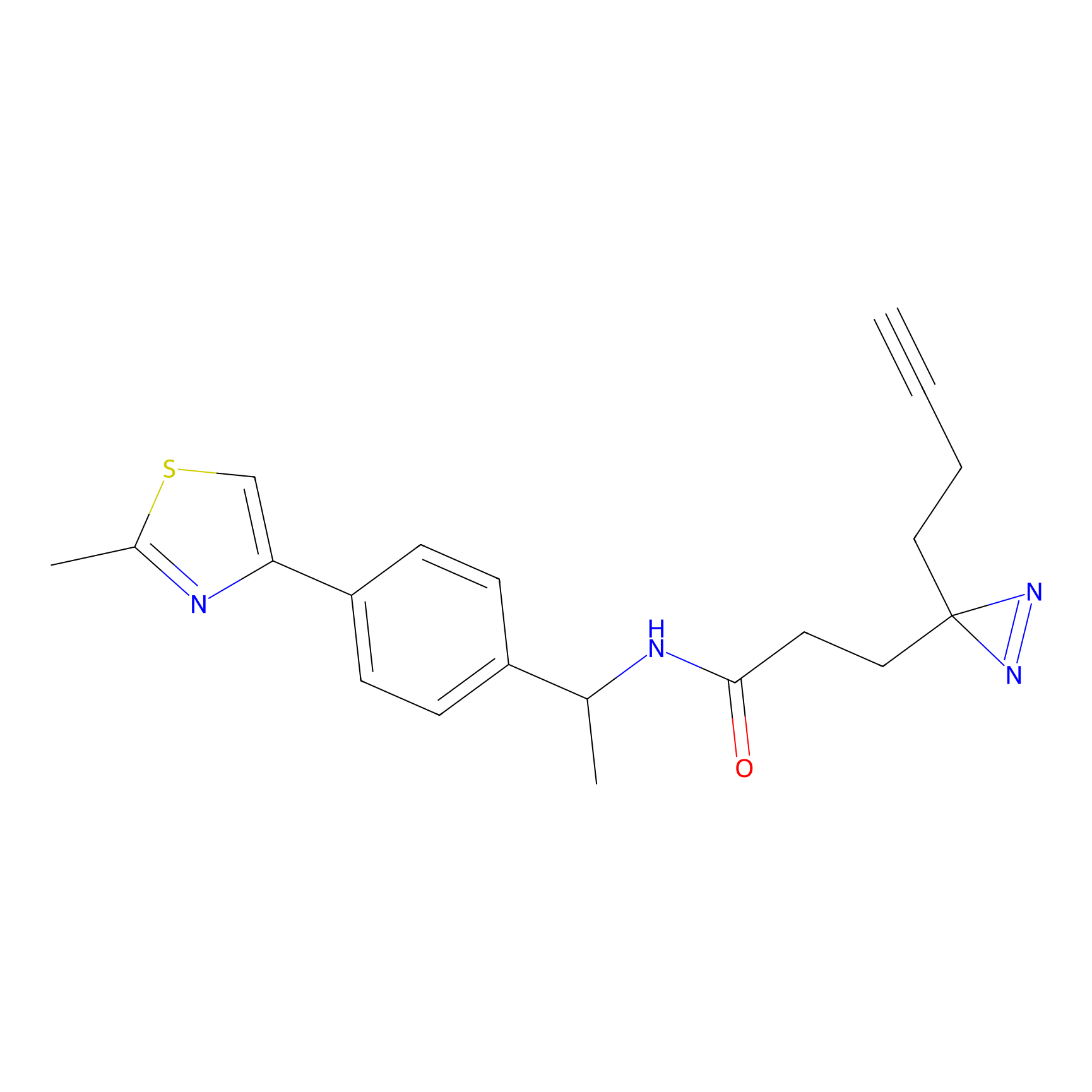
|
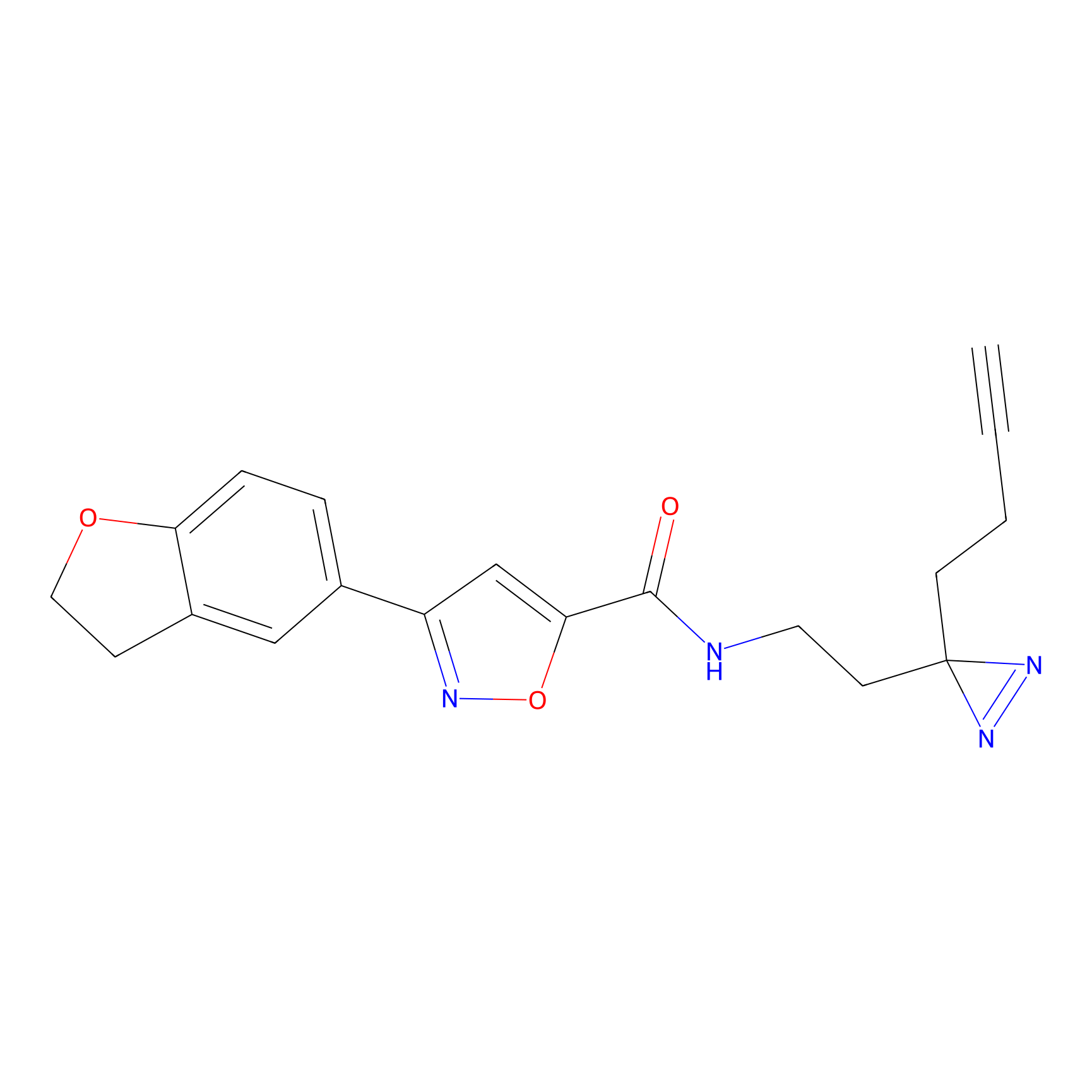
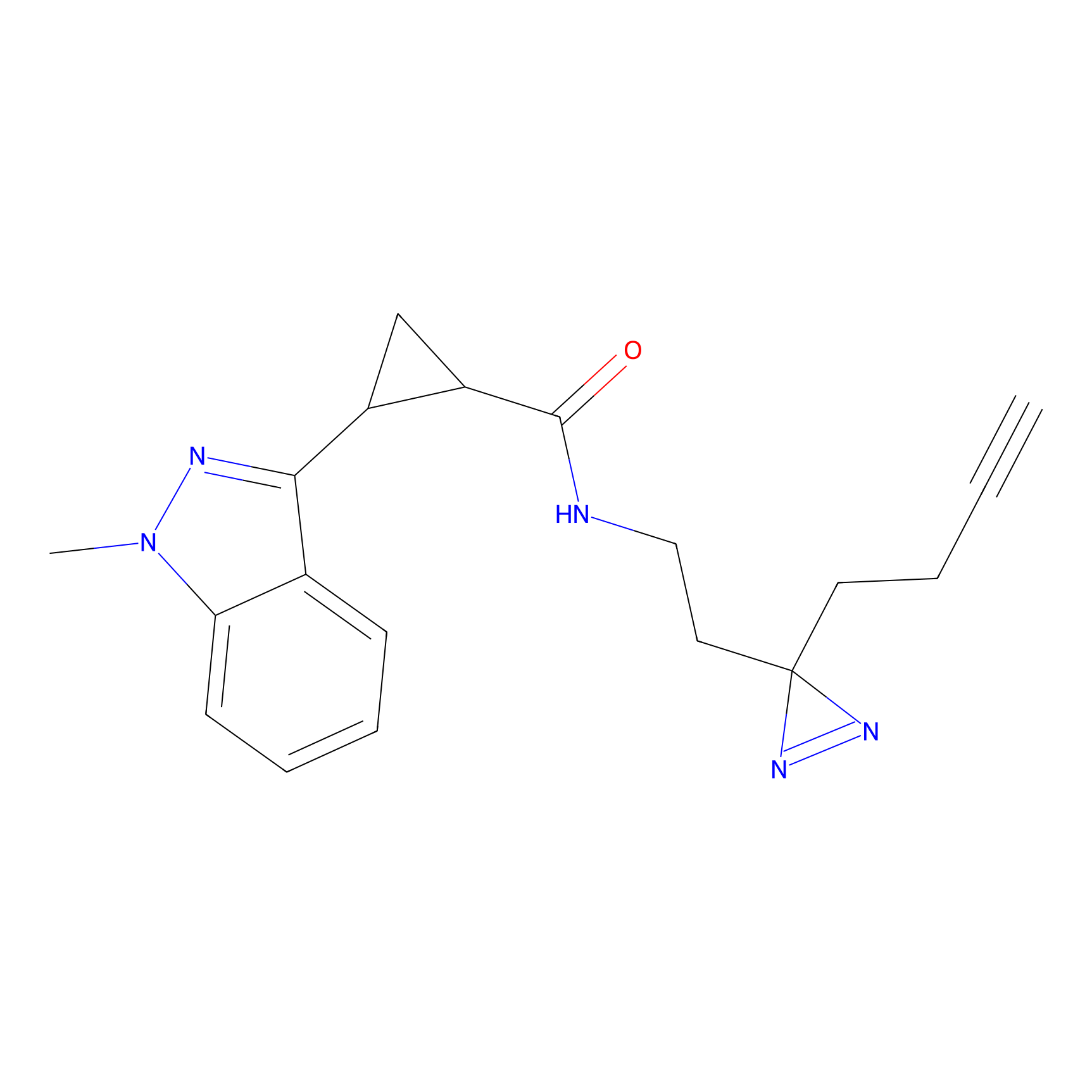
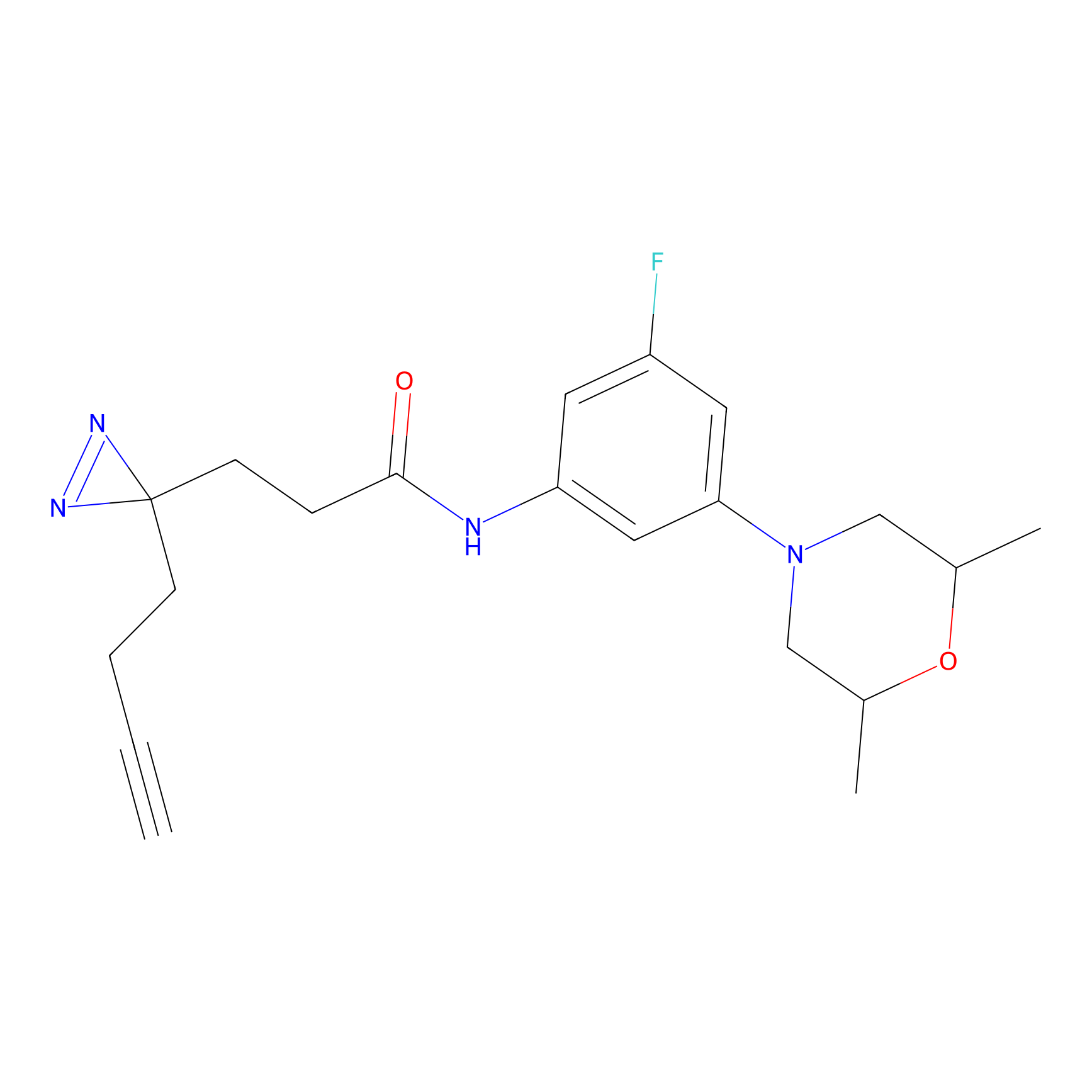
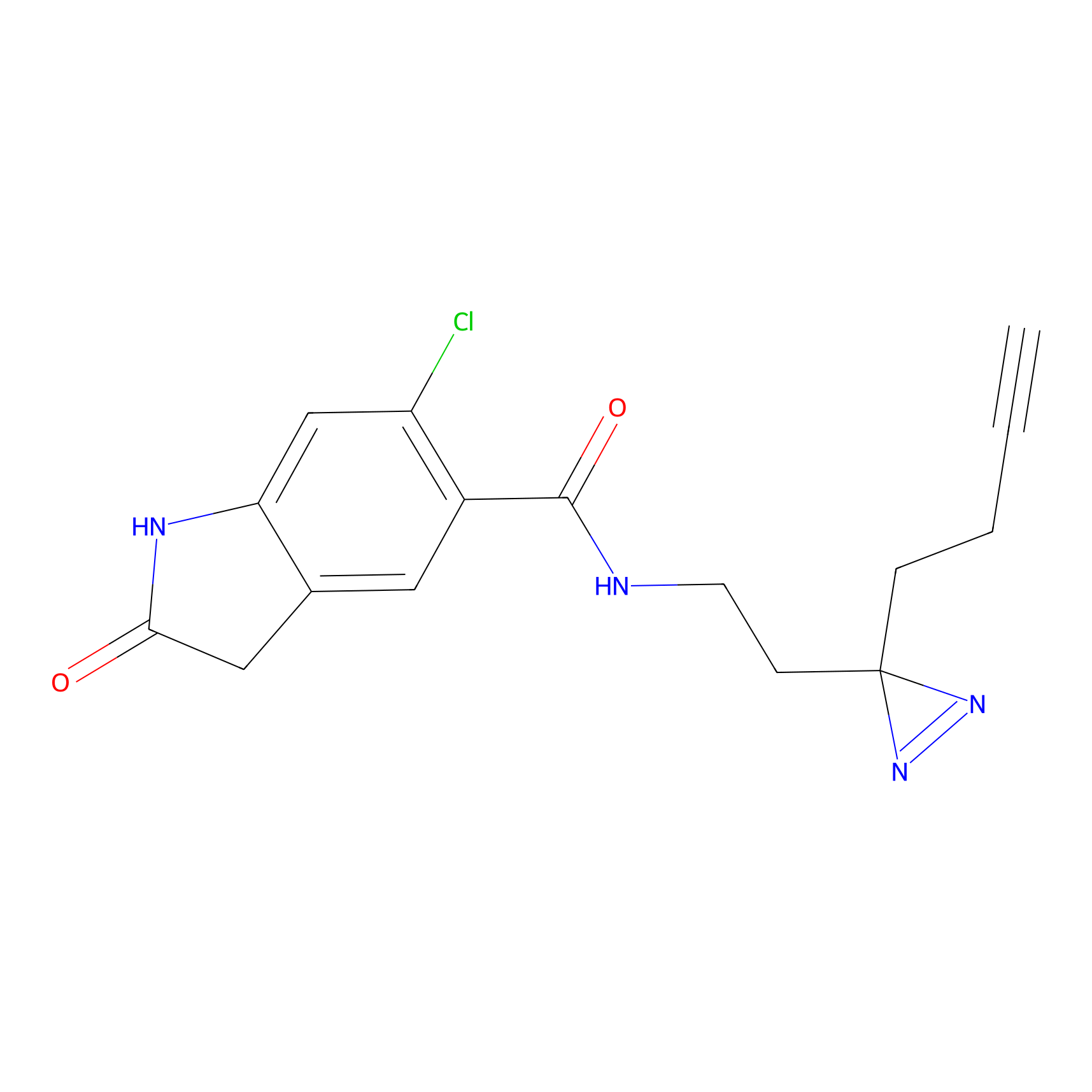
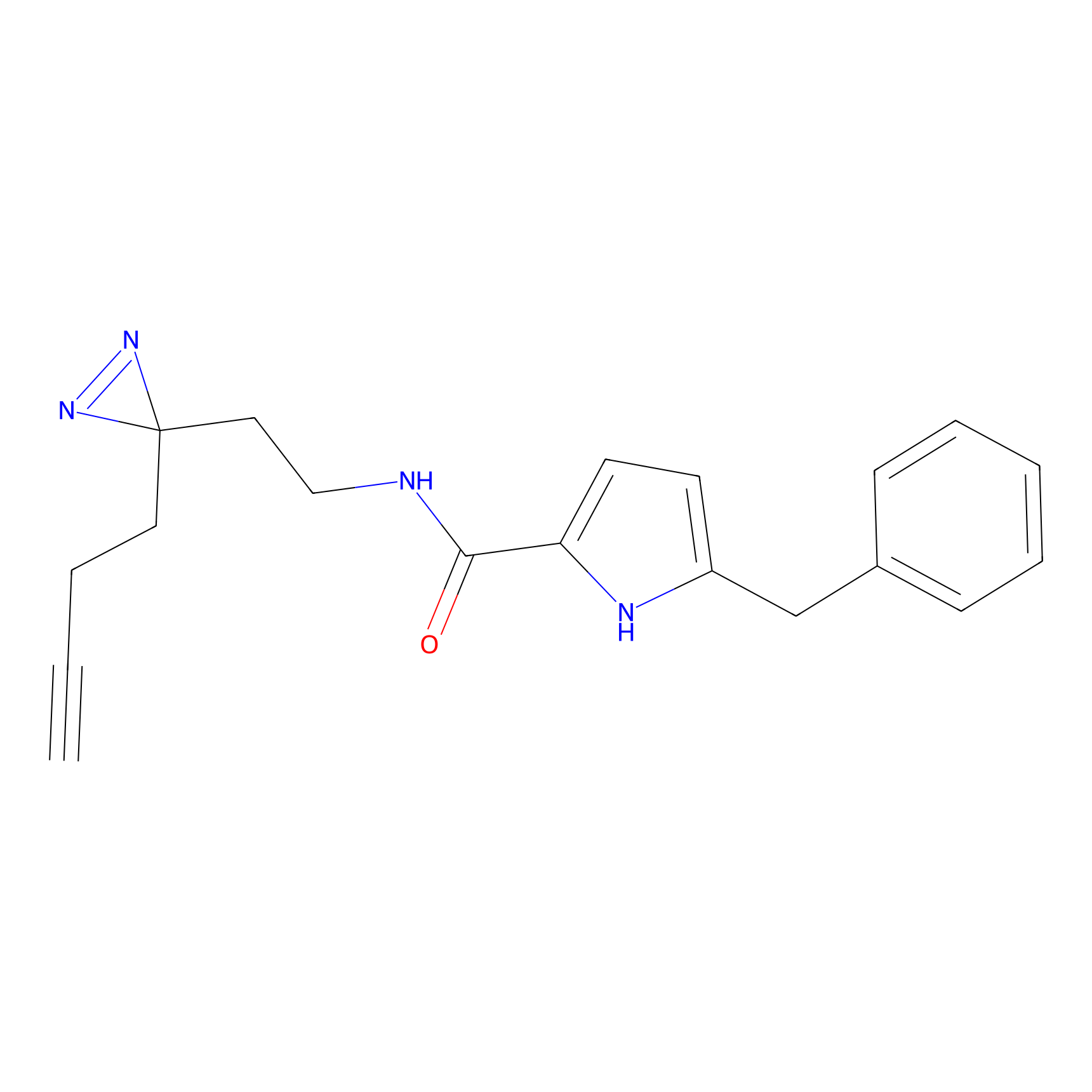
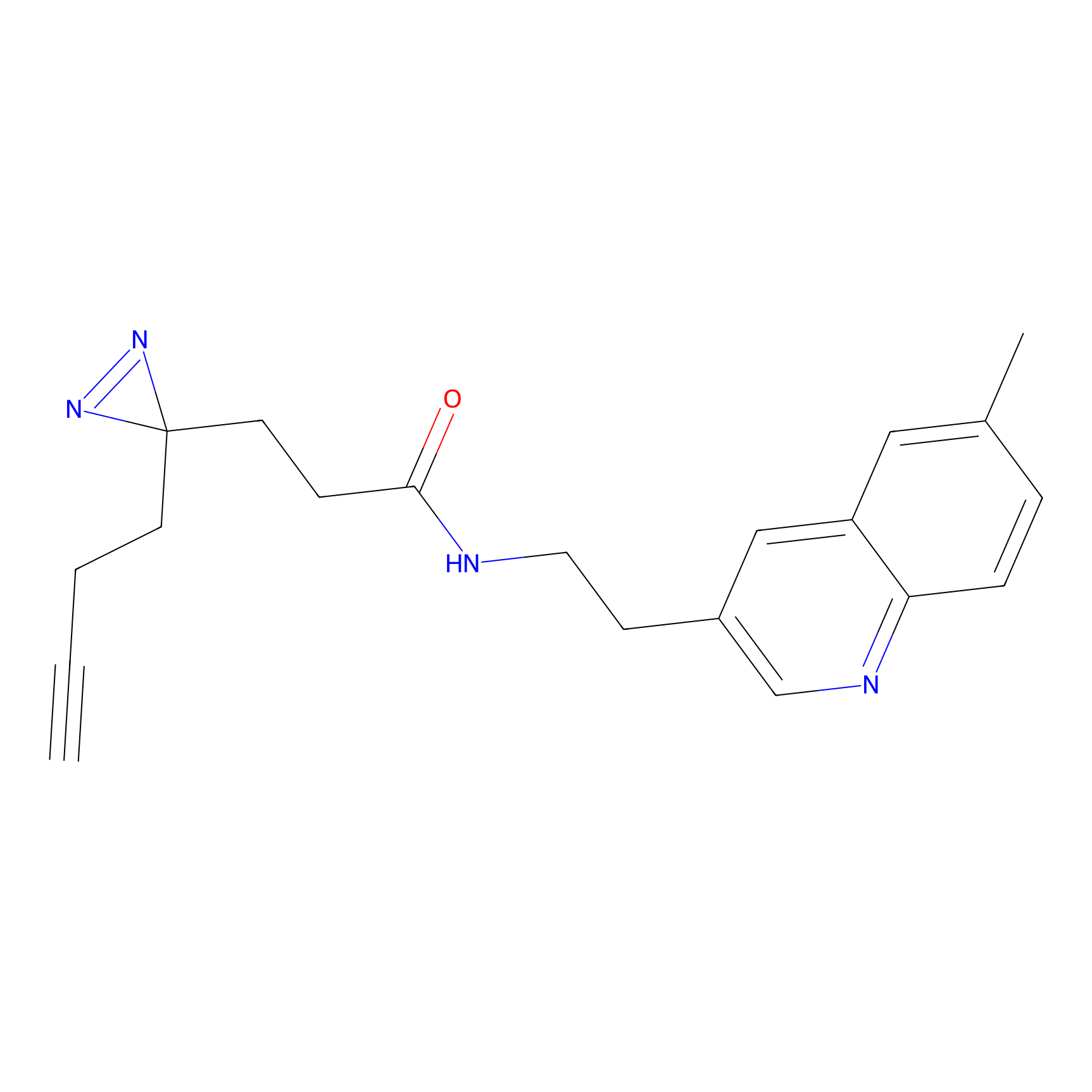
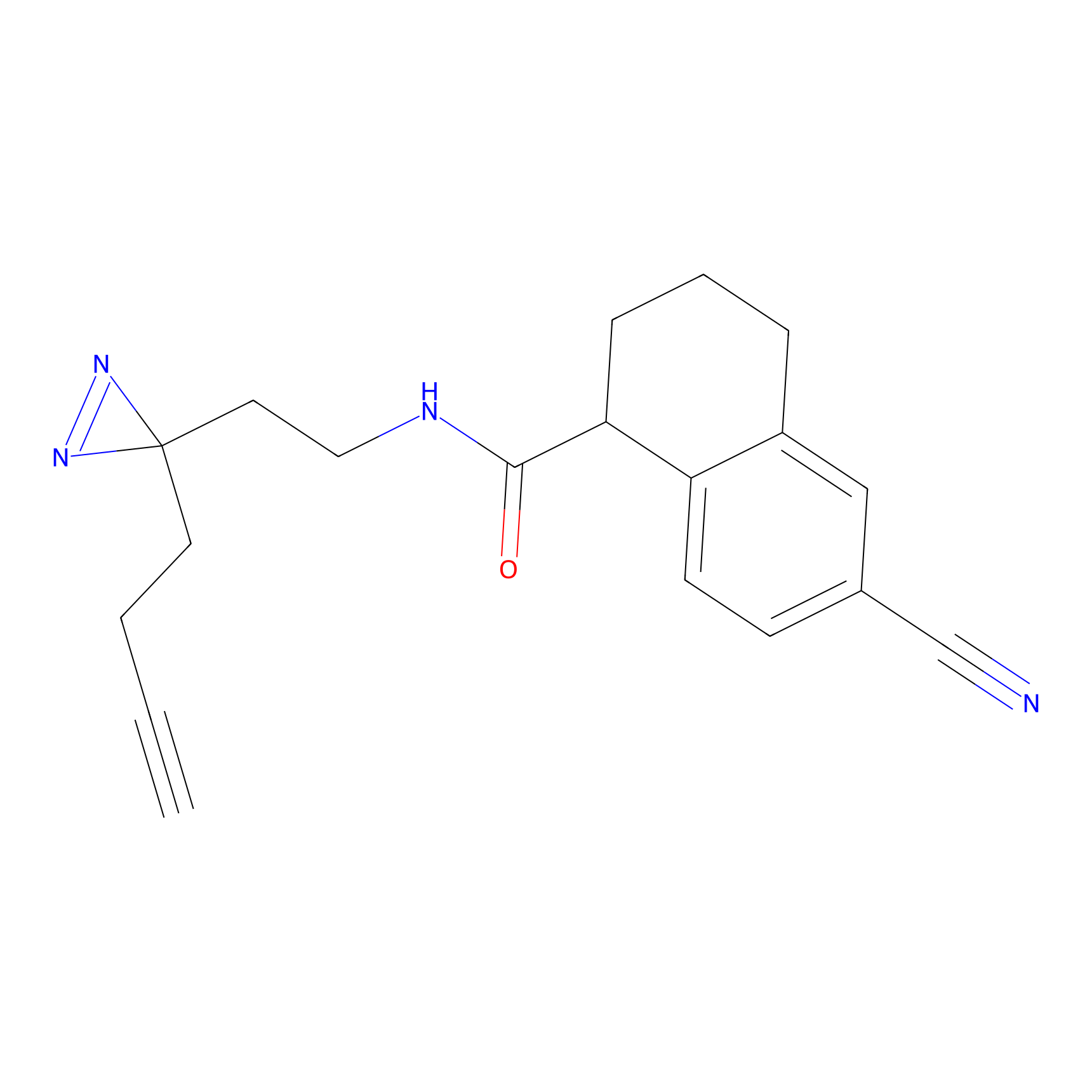
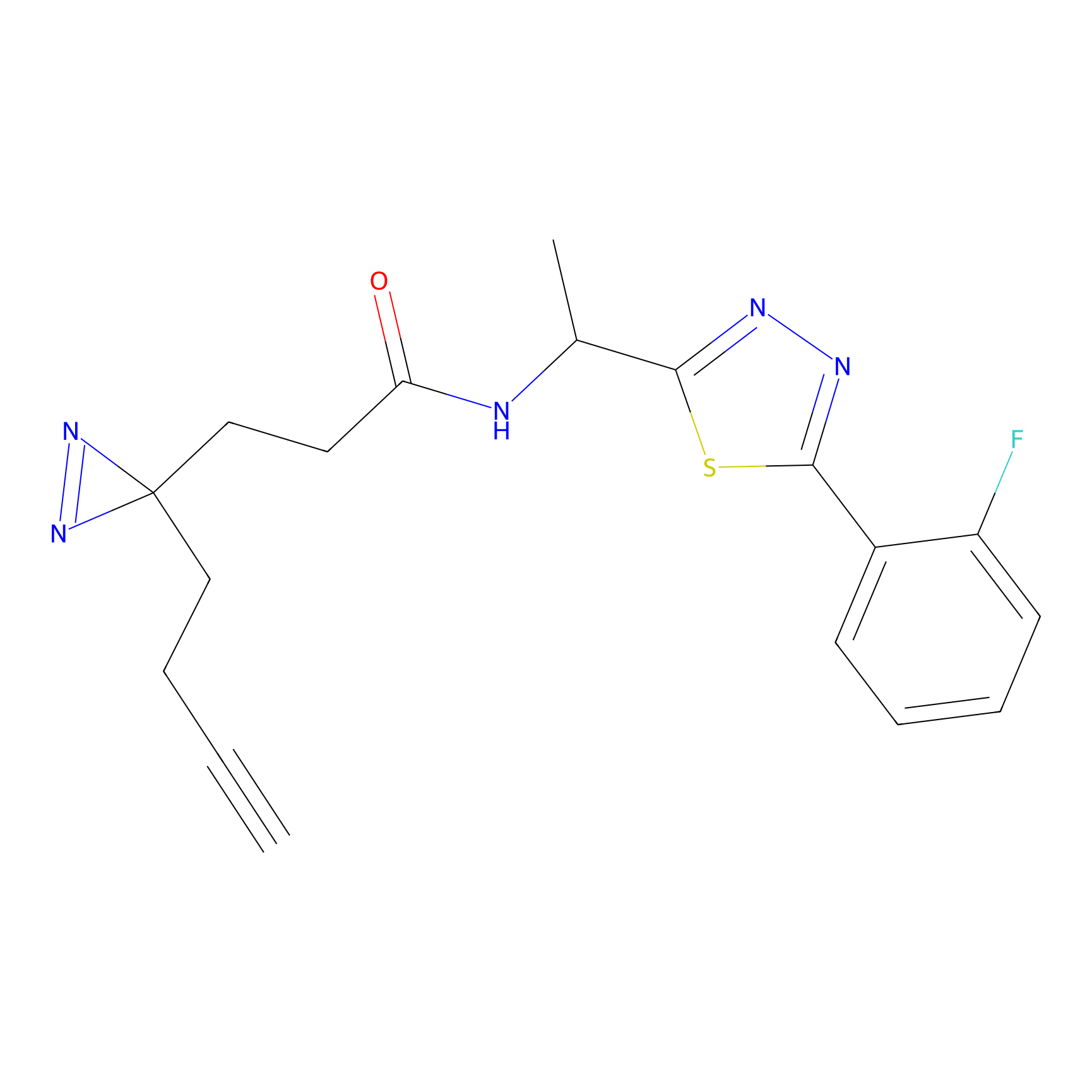
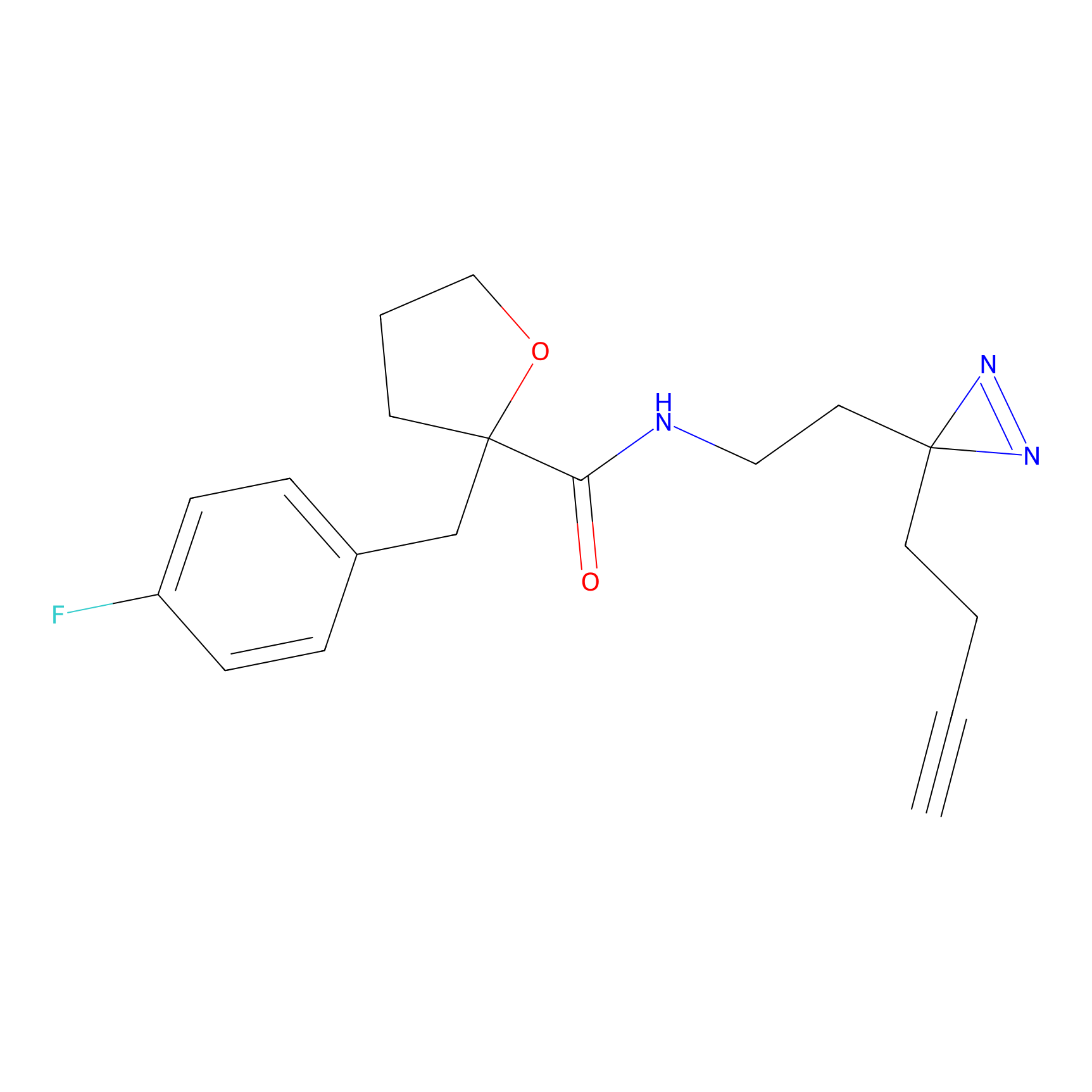
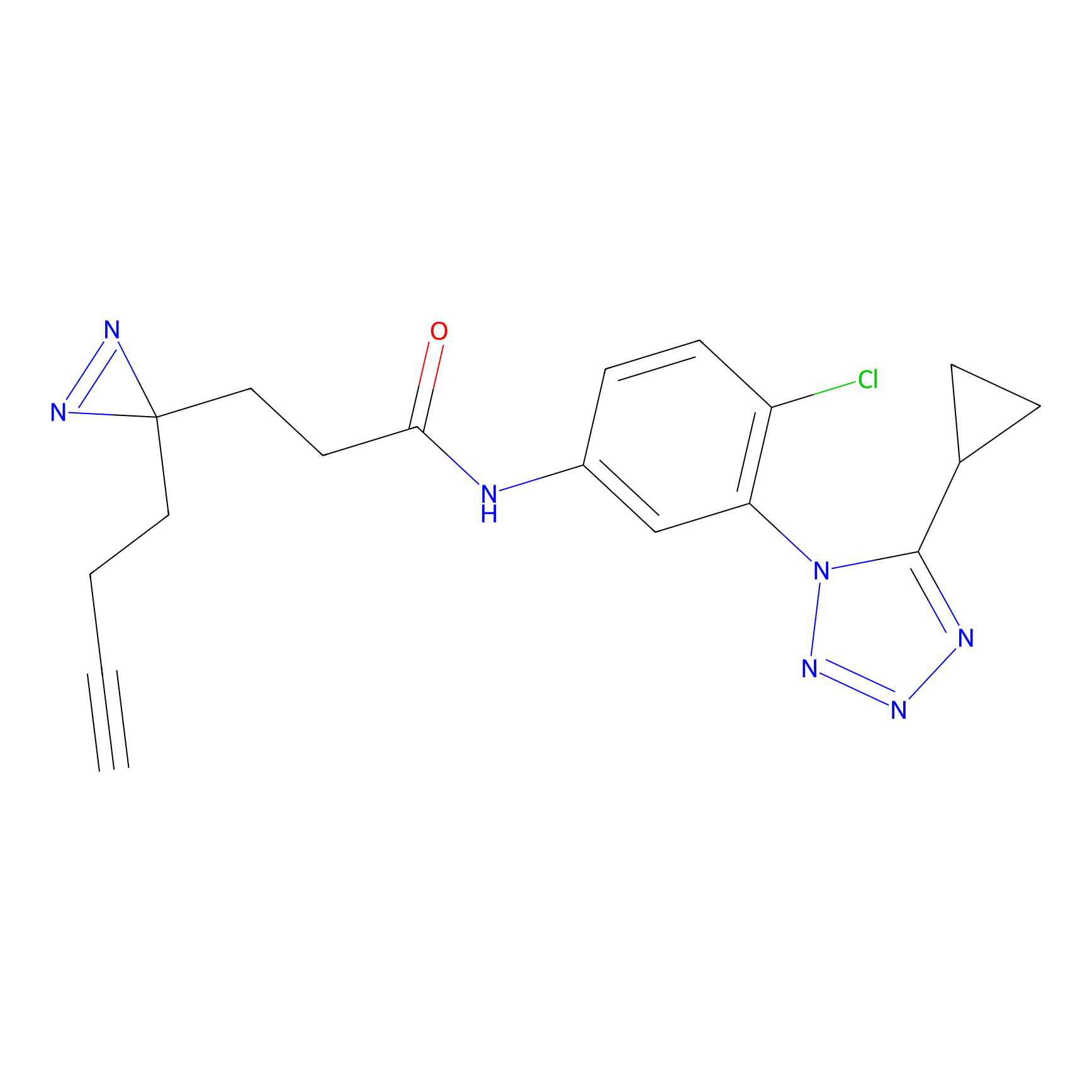
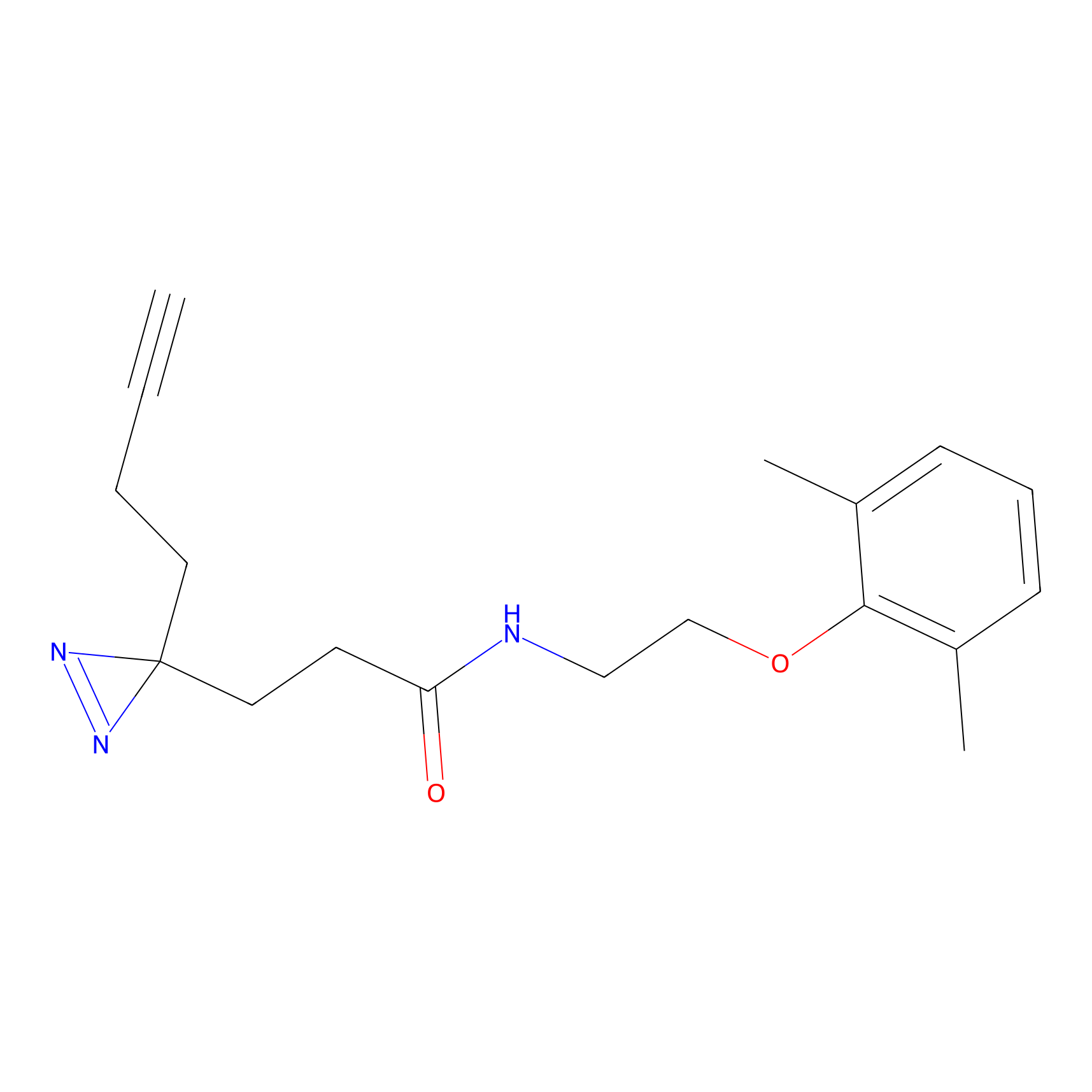
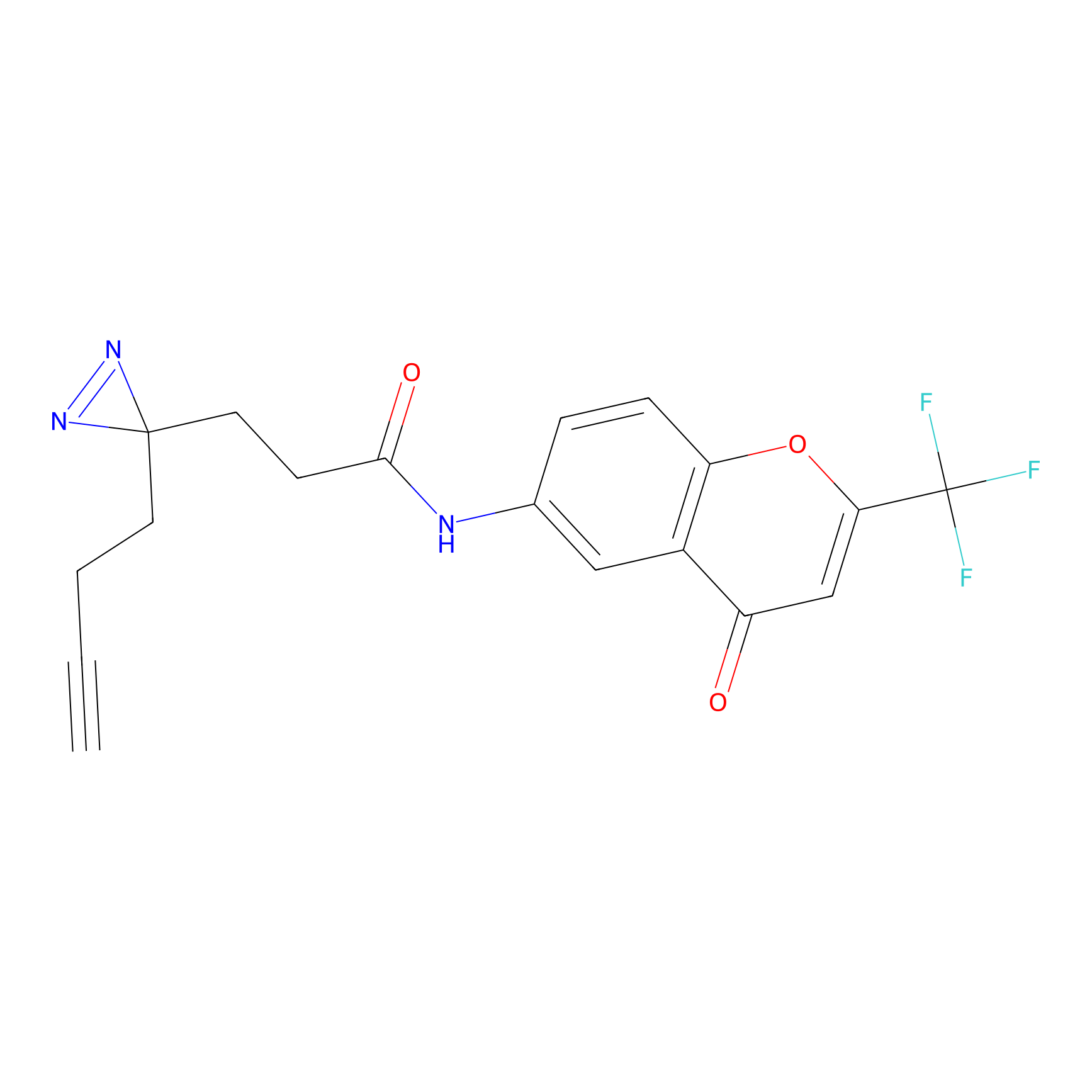
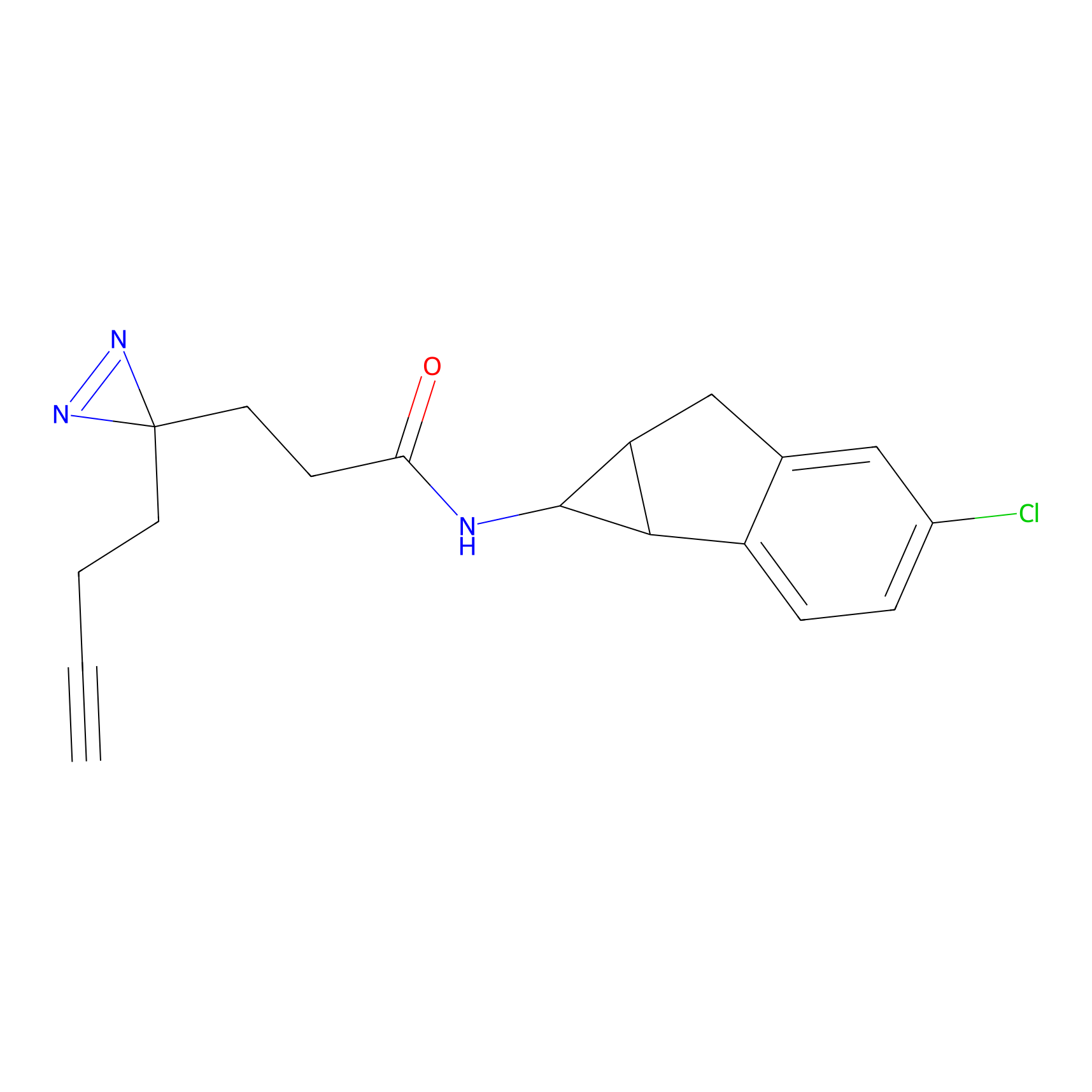
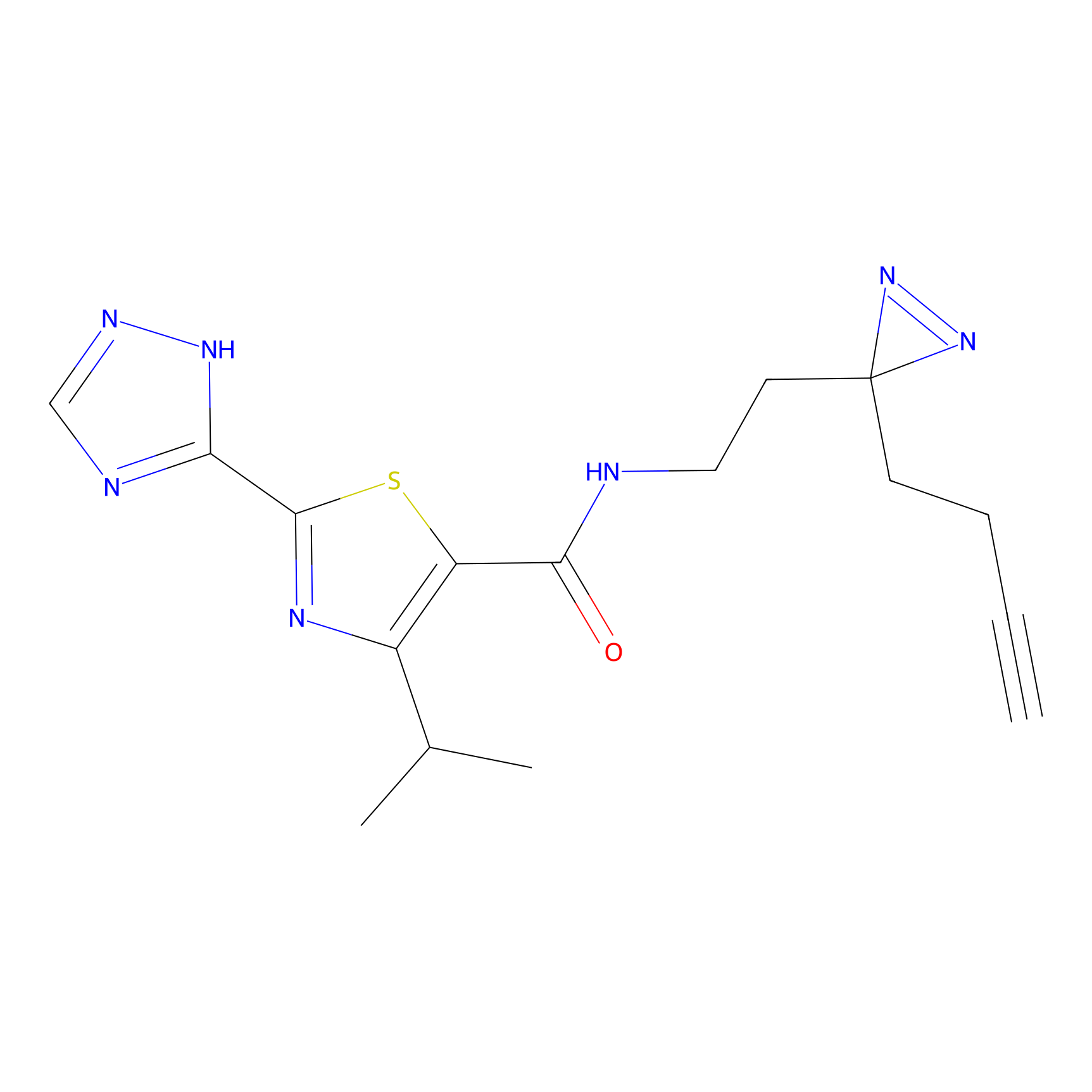
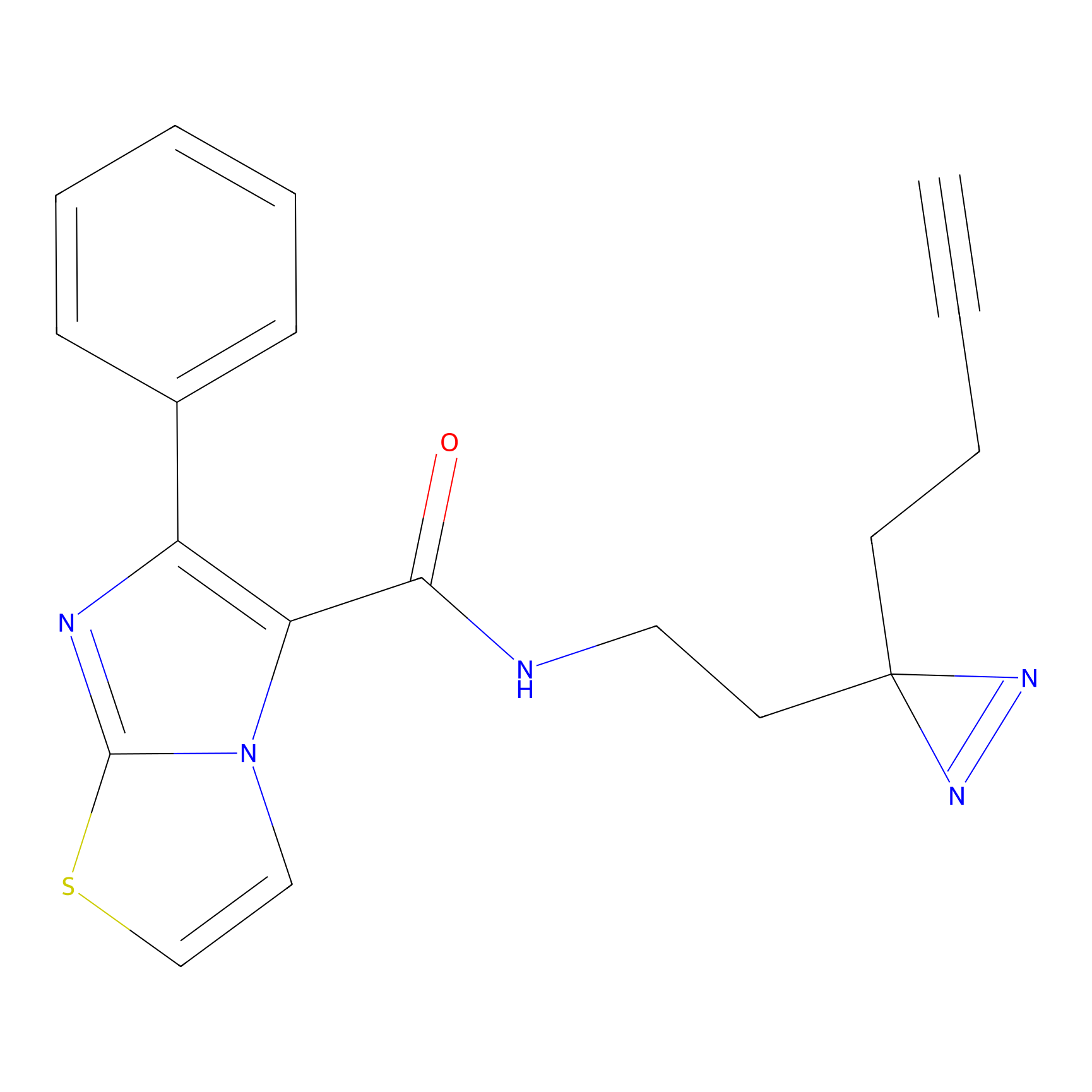
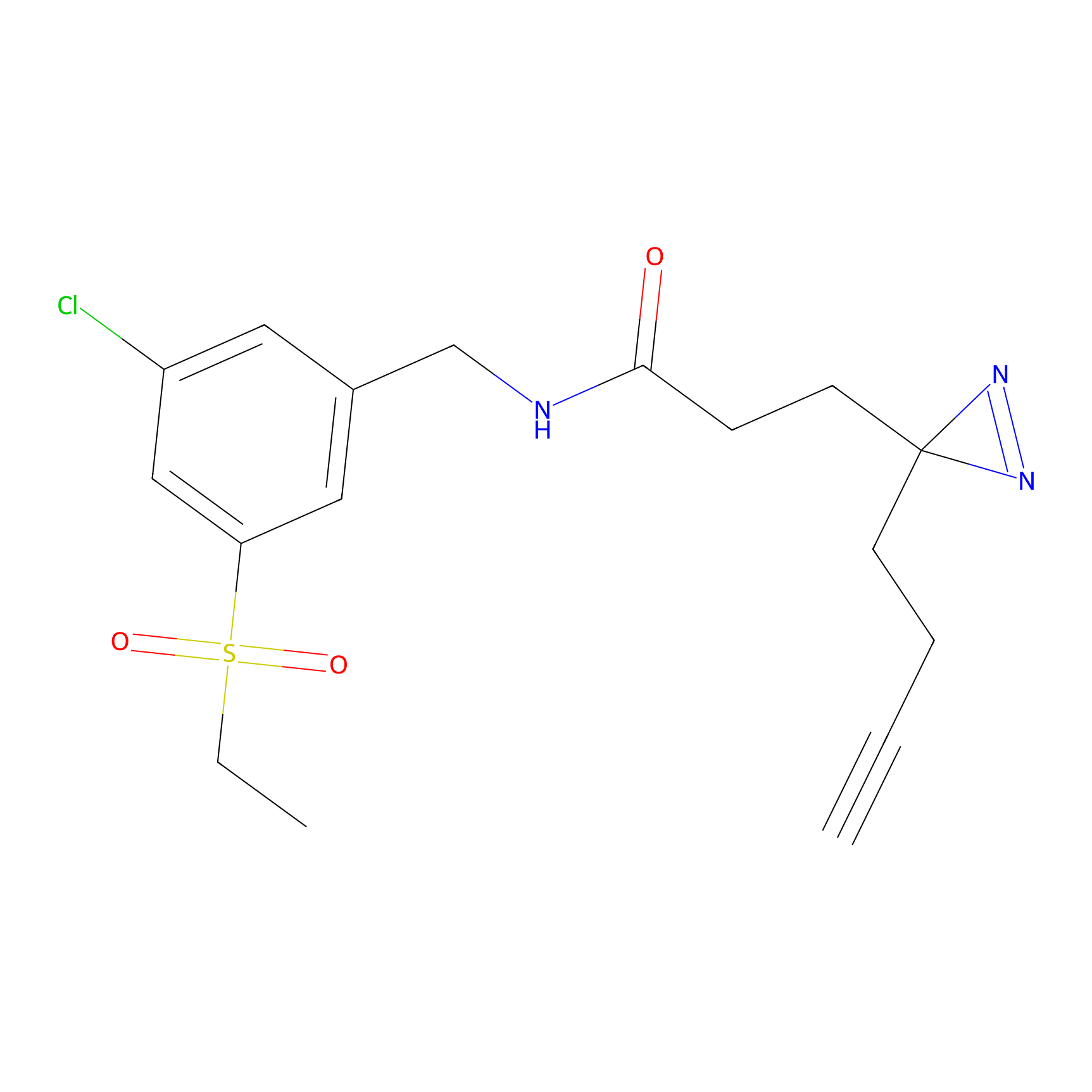
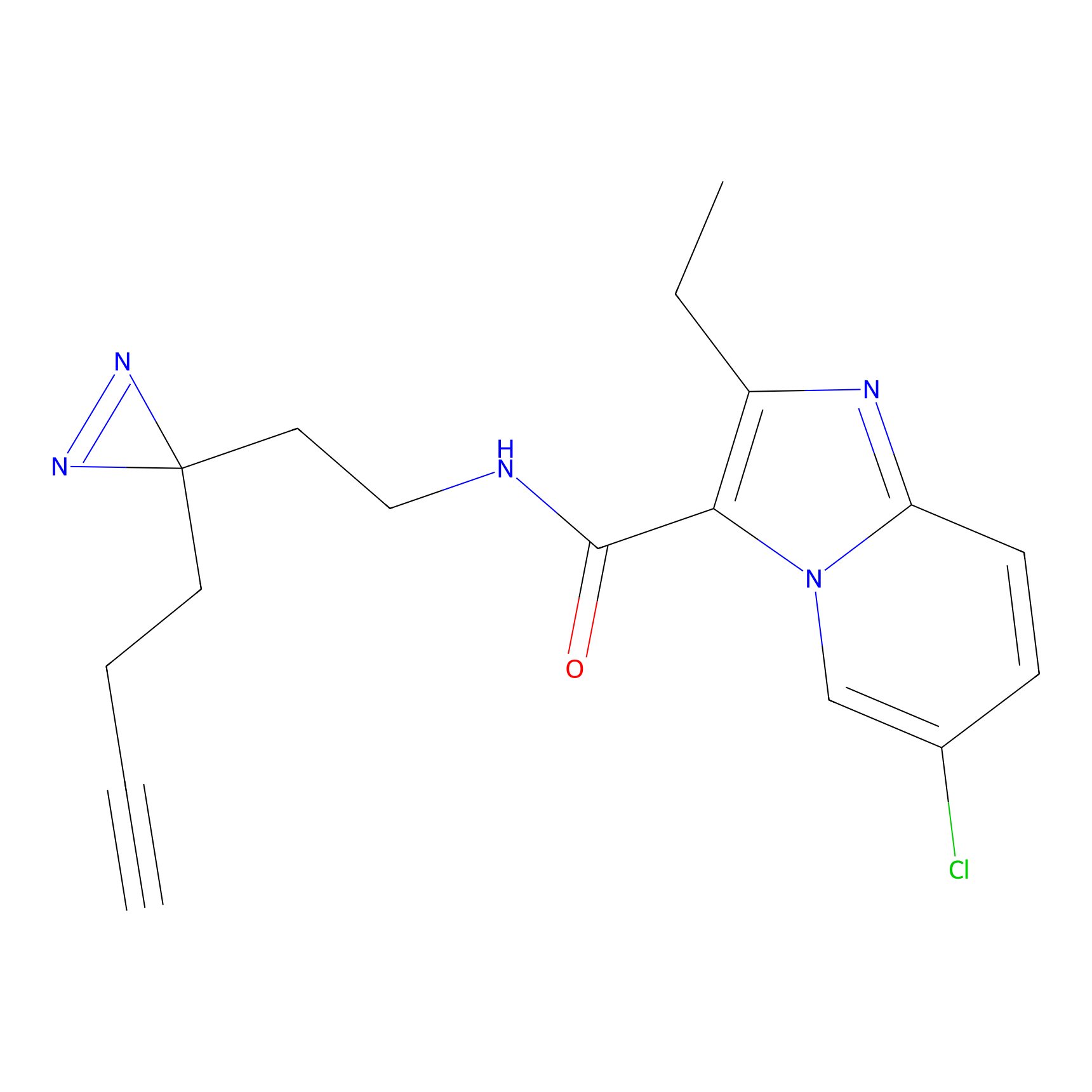
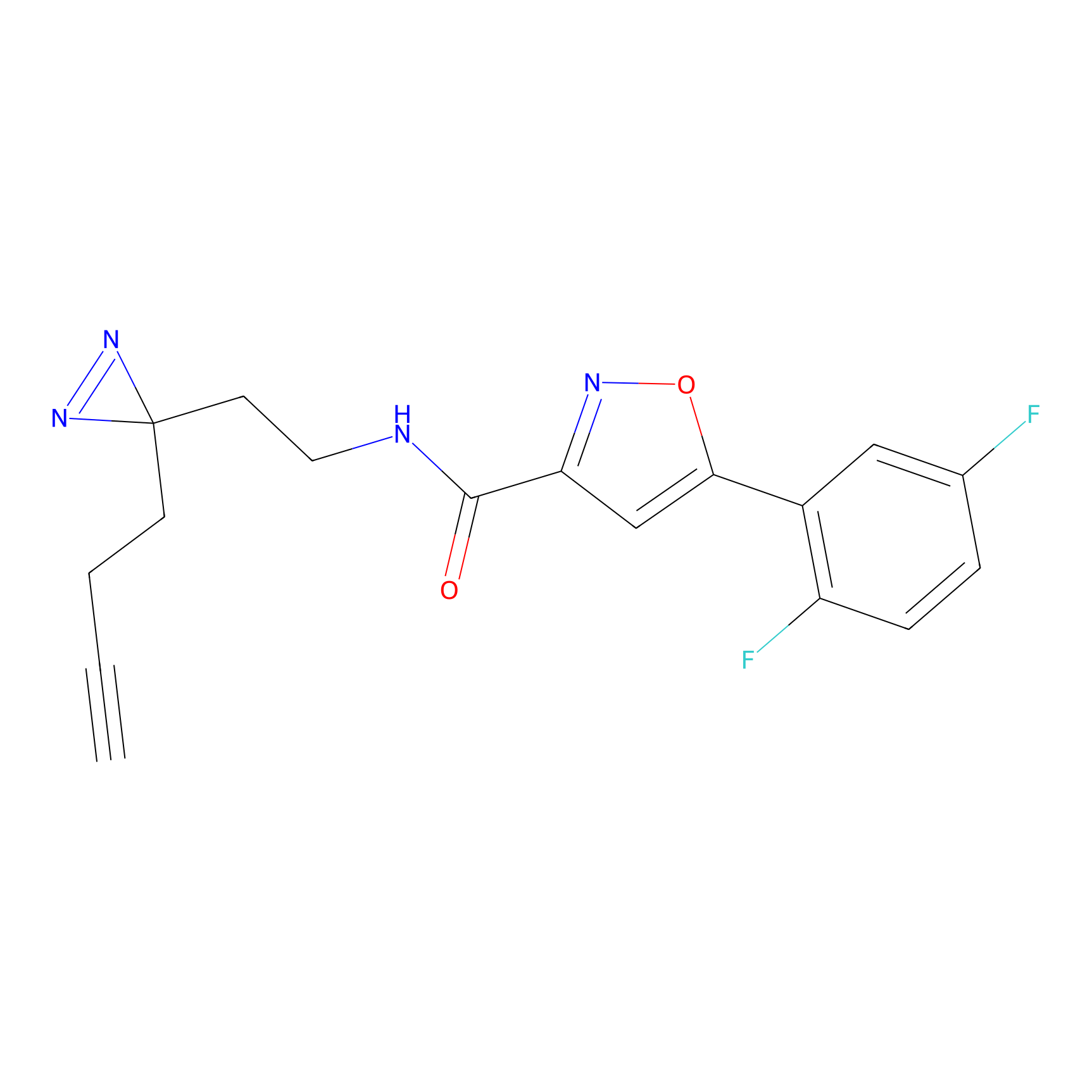
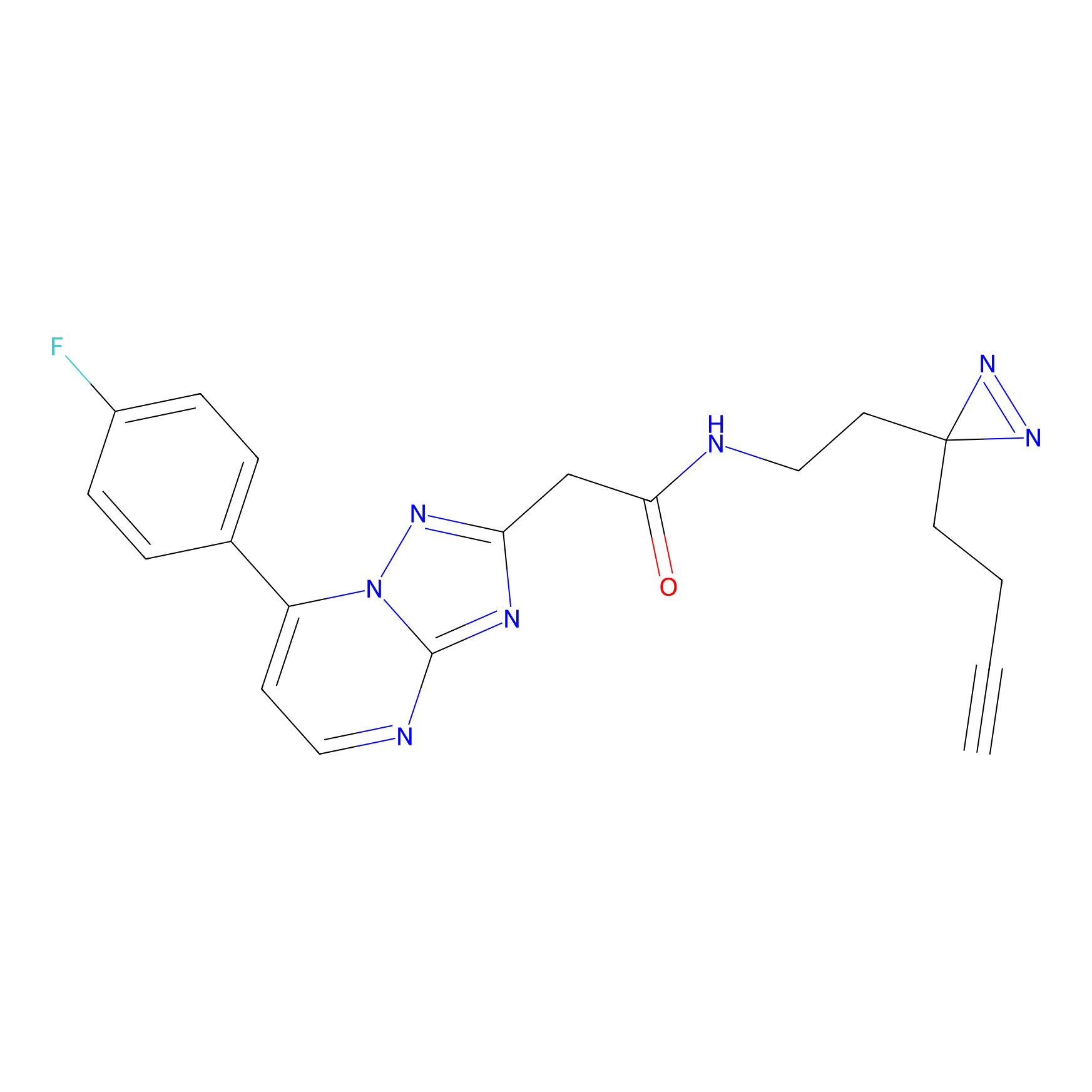
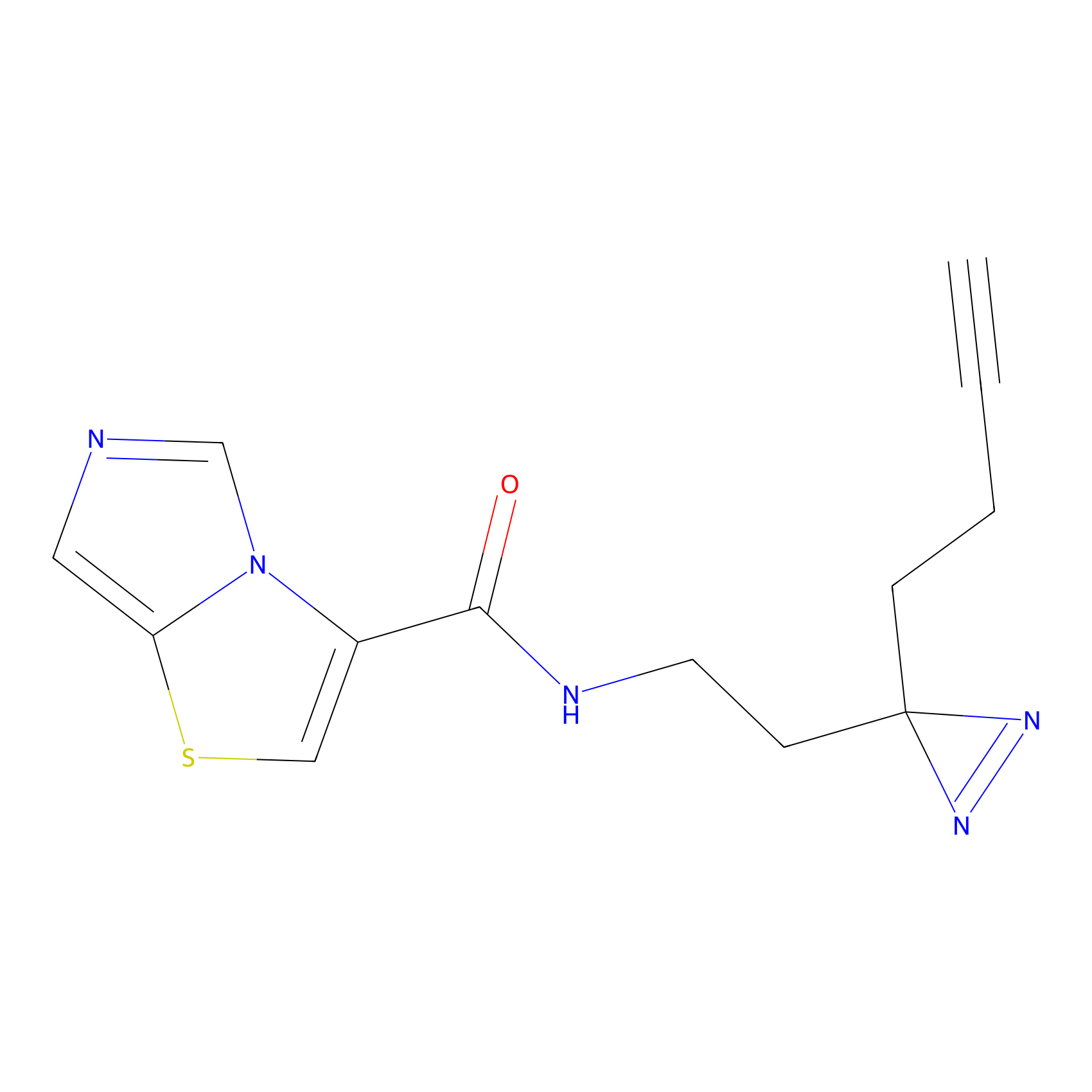
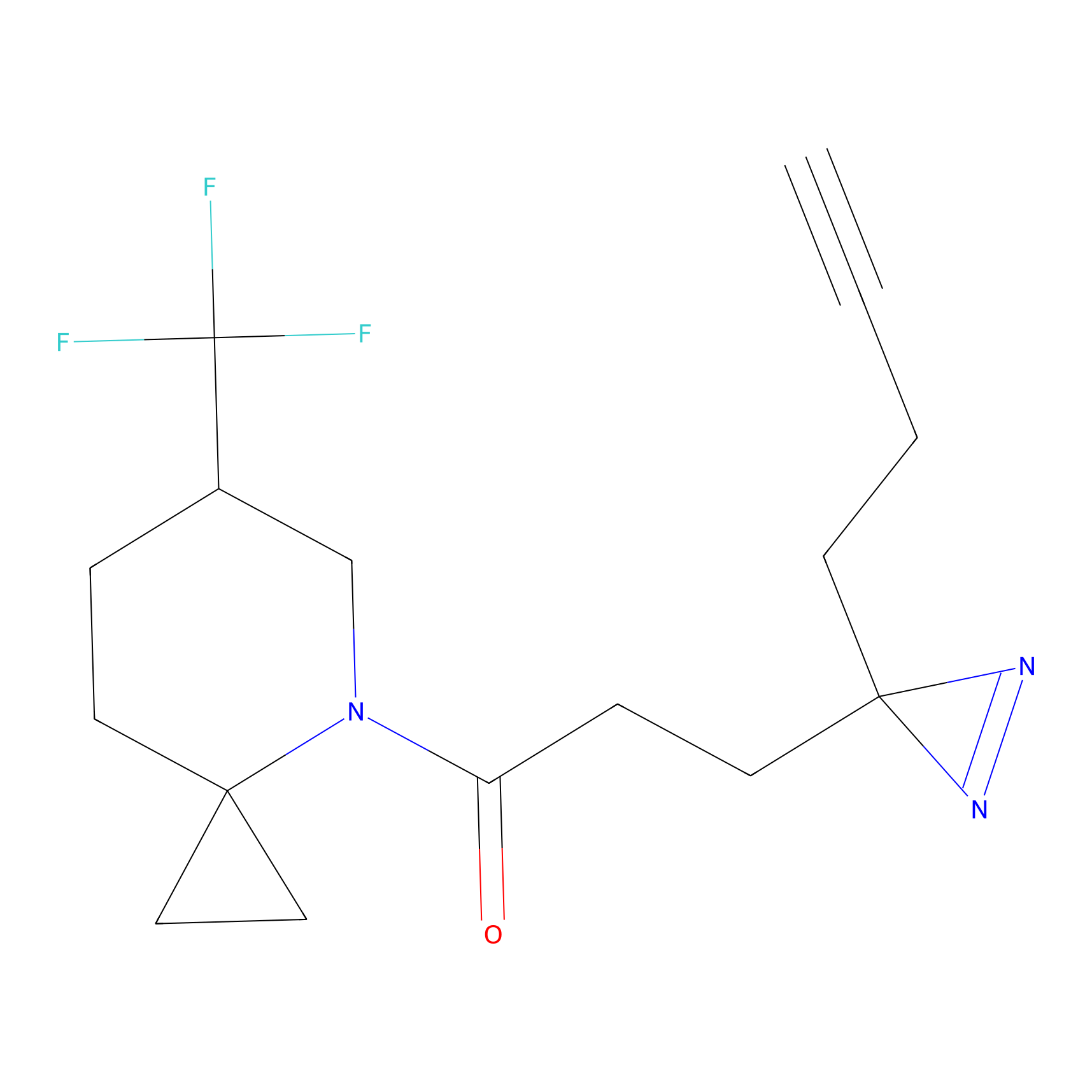
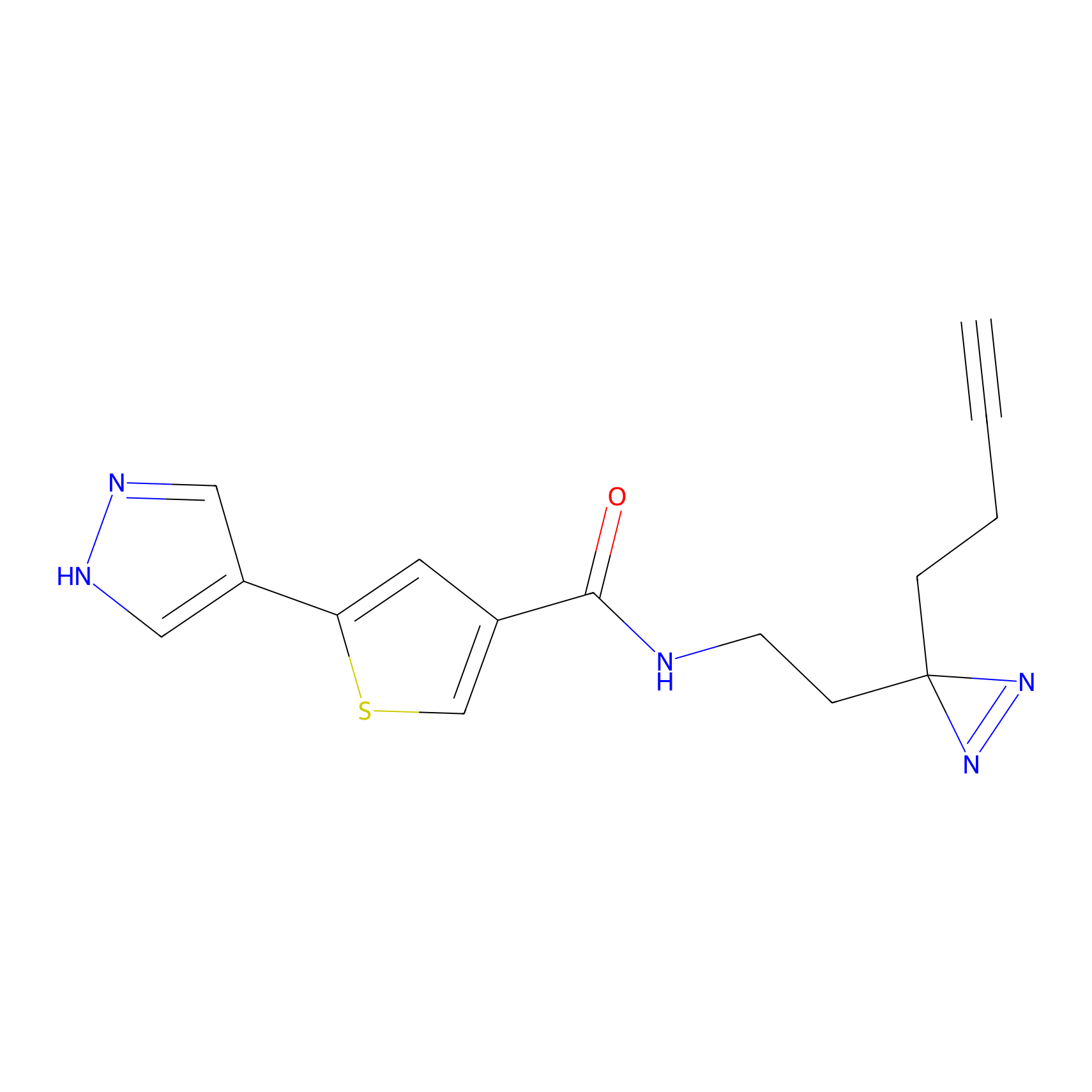
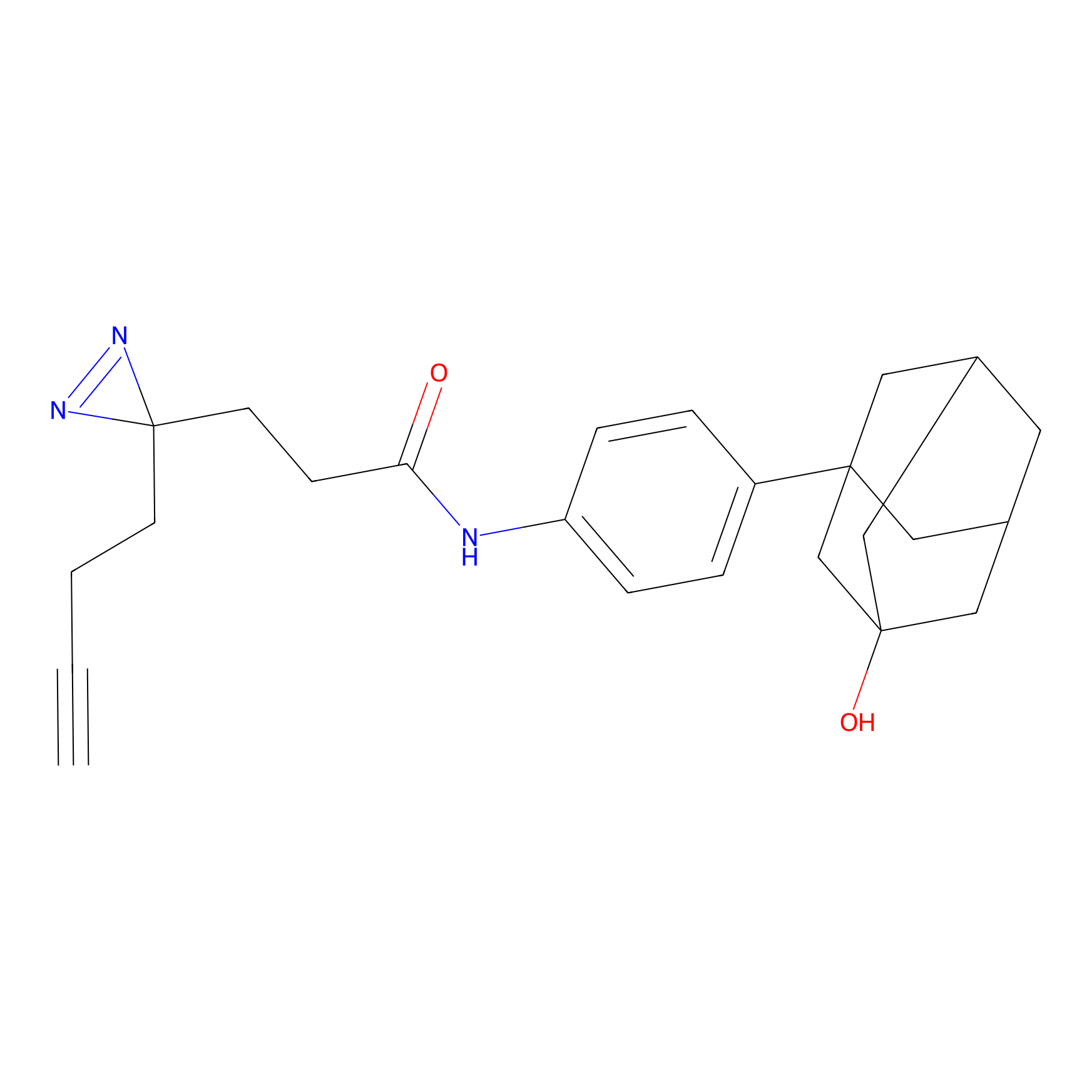
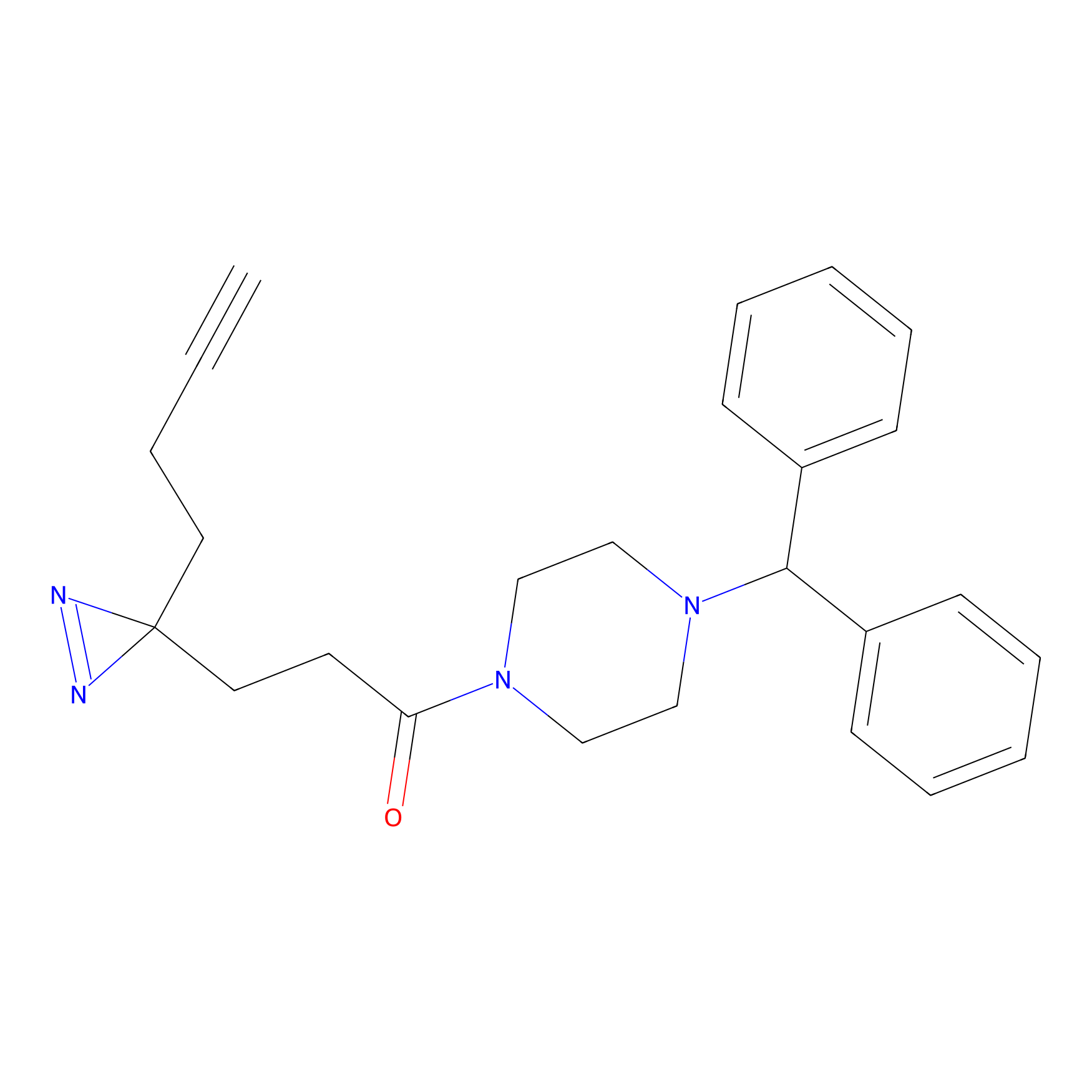
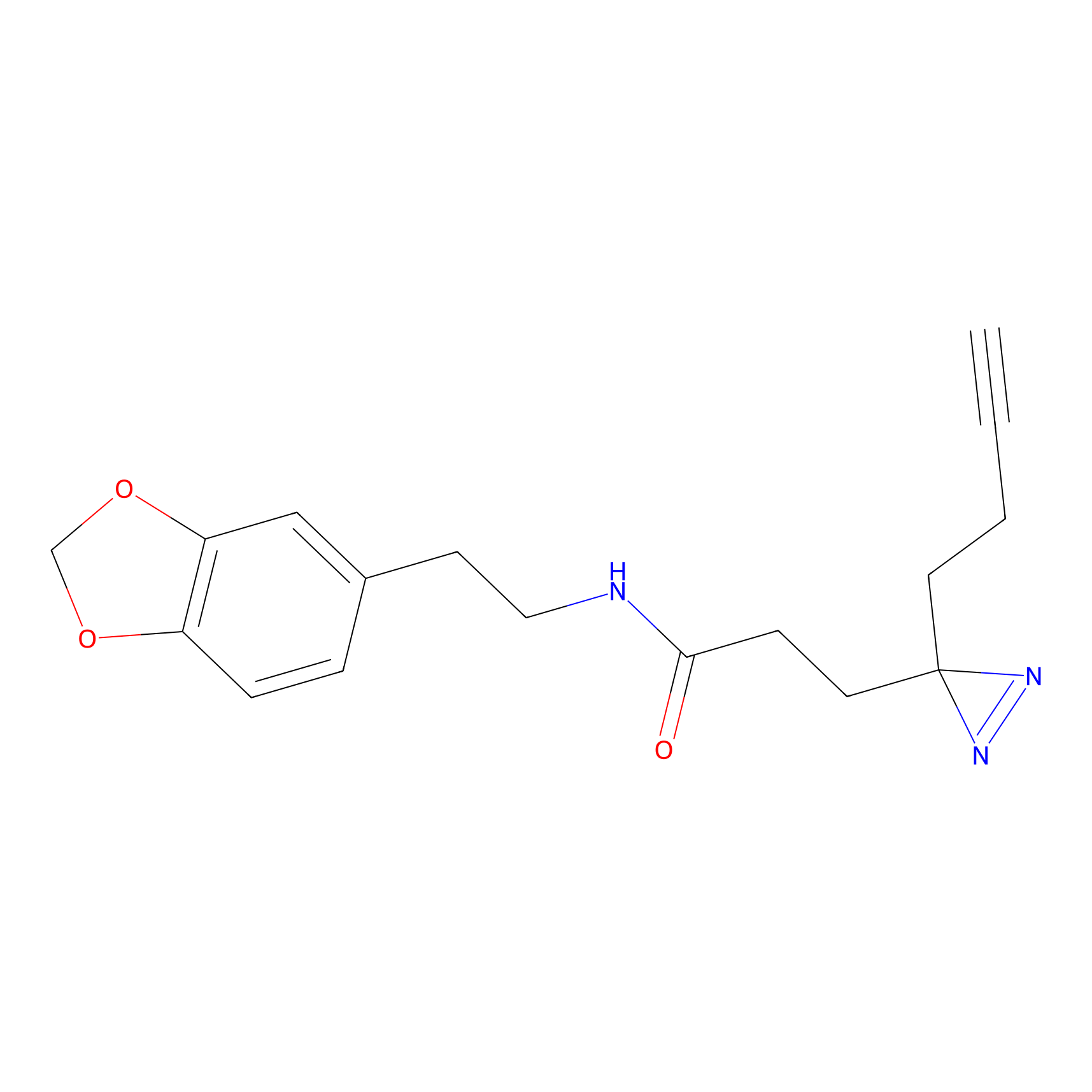
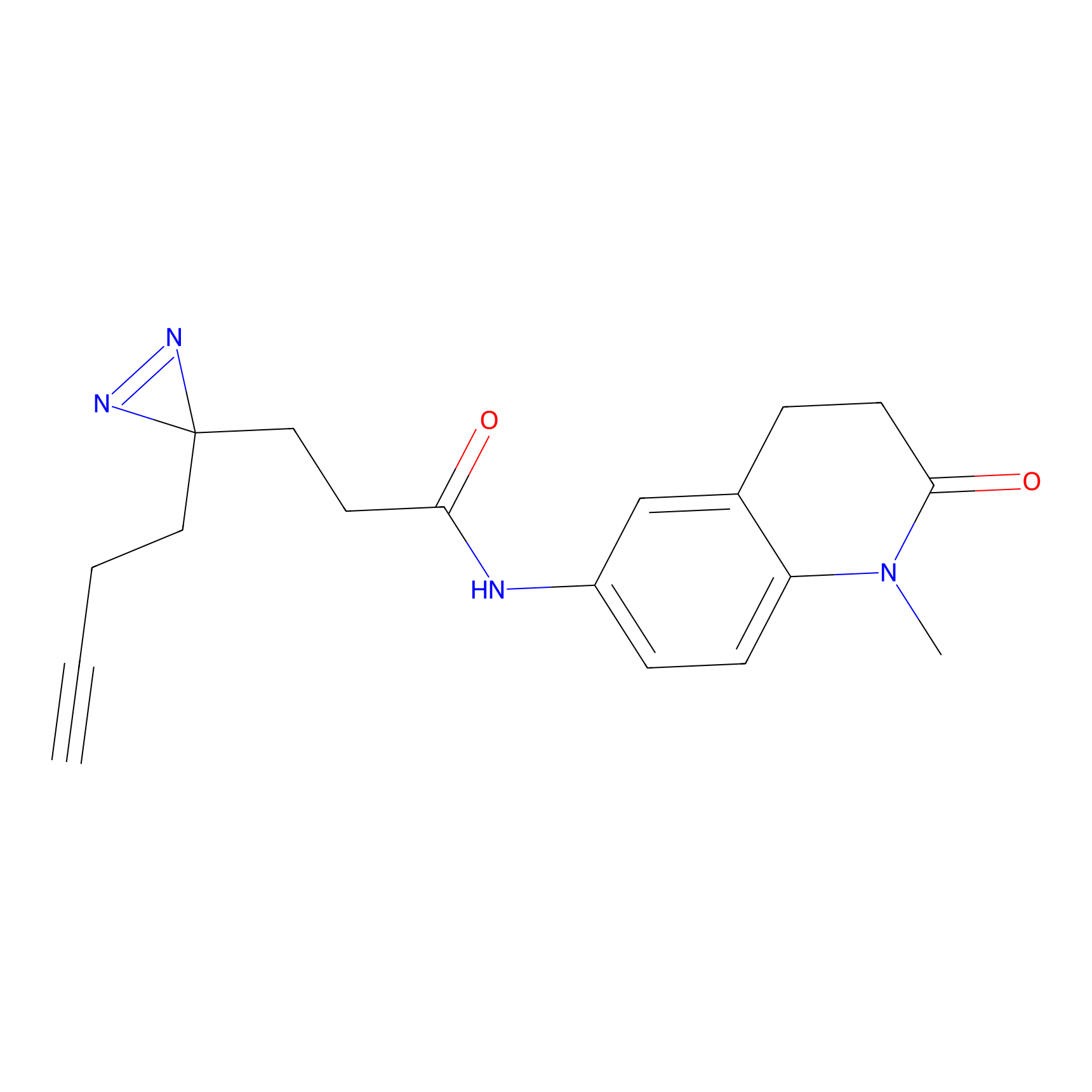
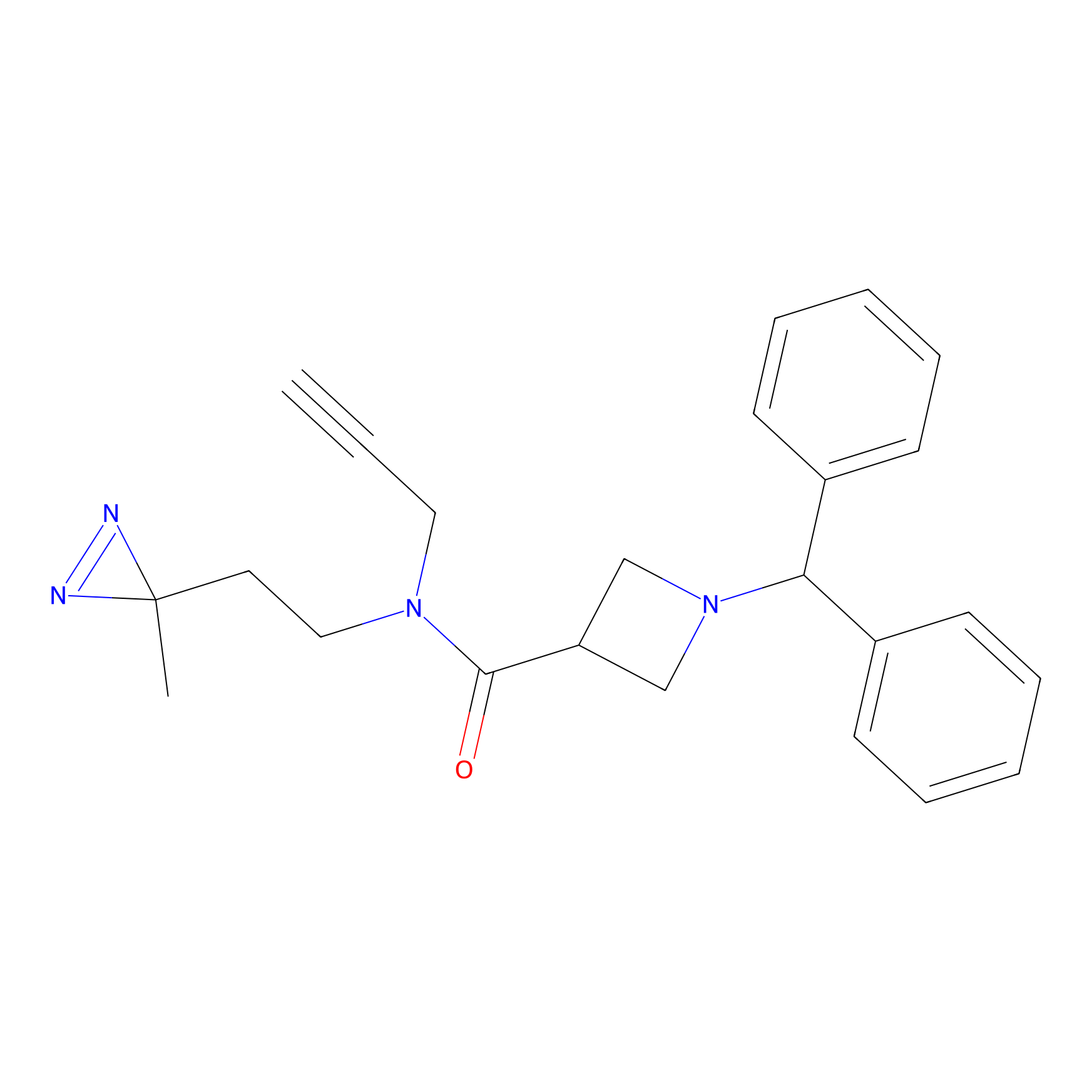
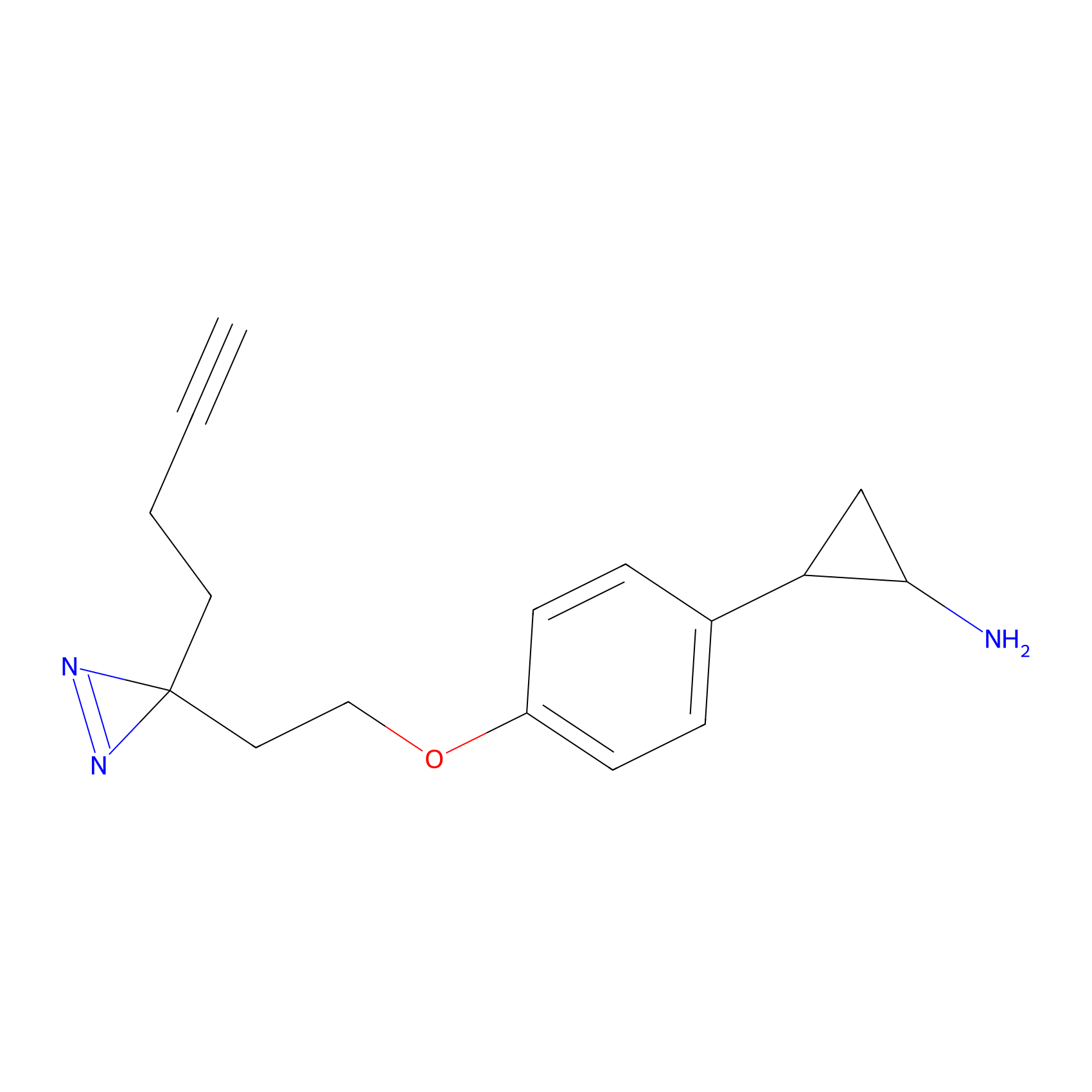
STPyne Probe Info |
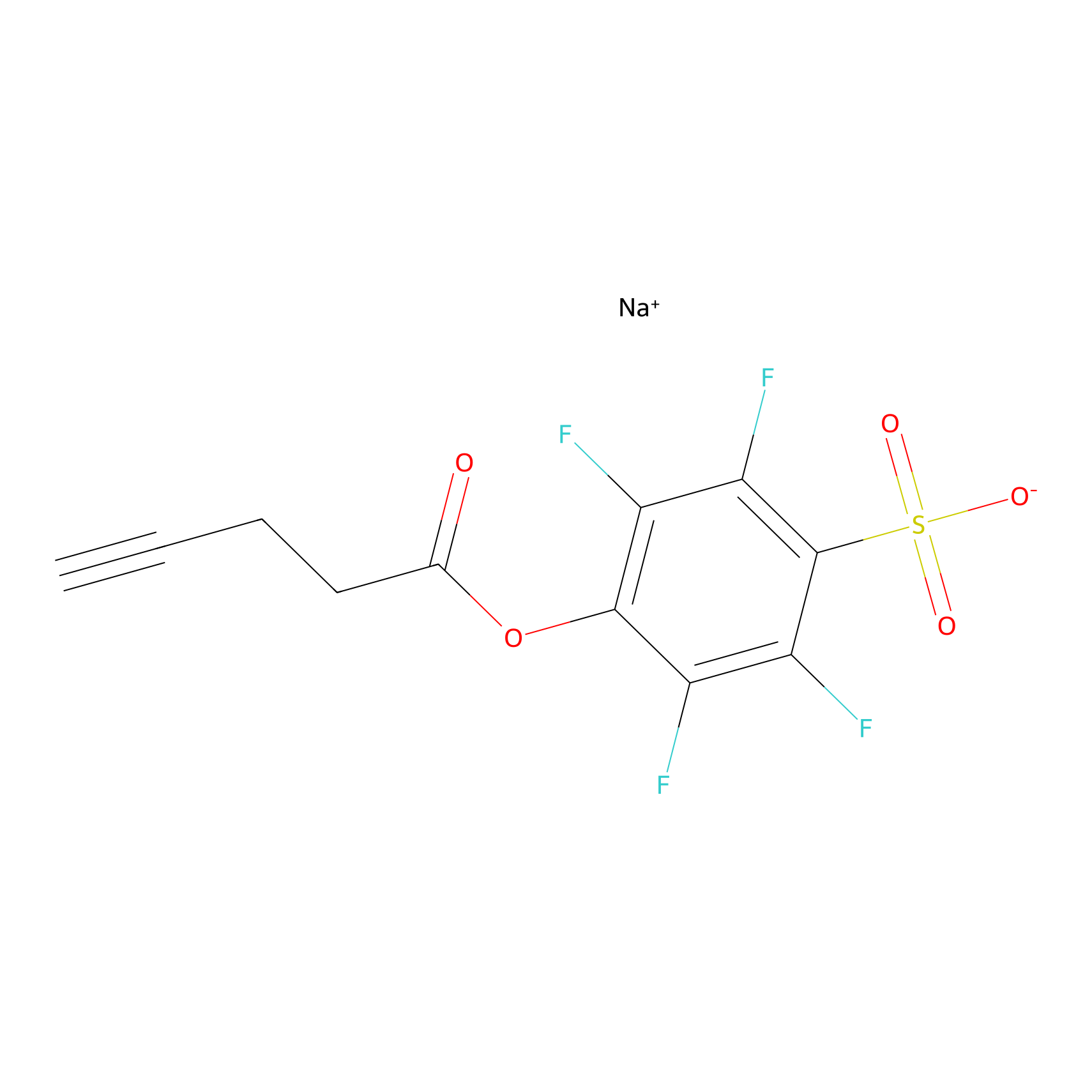 |
K153(3.34); K155(1.56); K56(0.80); K71(4.47) | LDD0277 | [3] | |
|
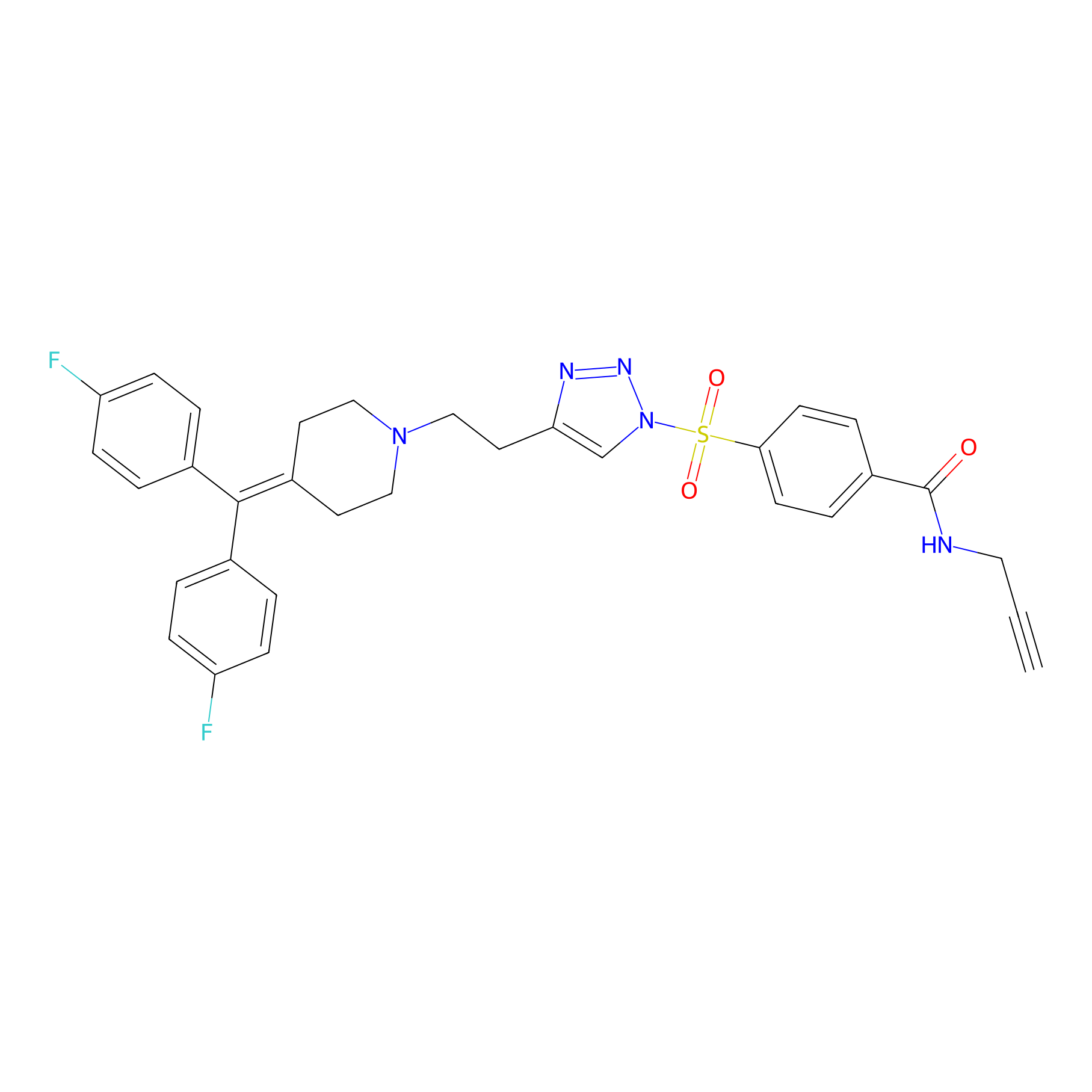
ONAyne Probe Info |
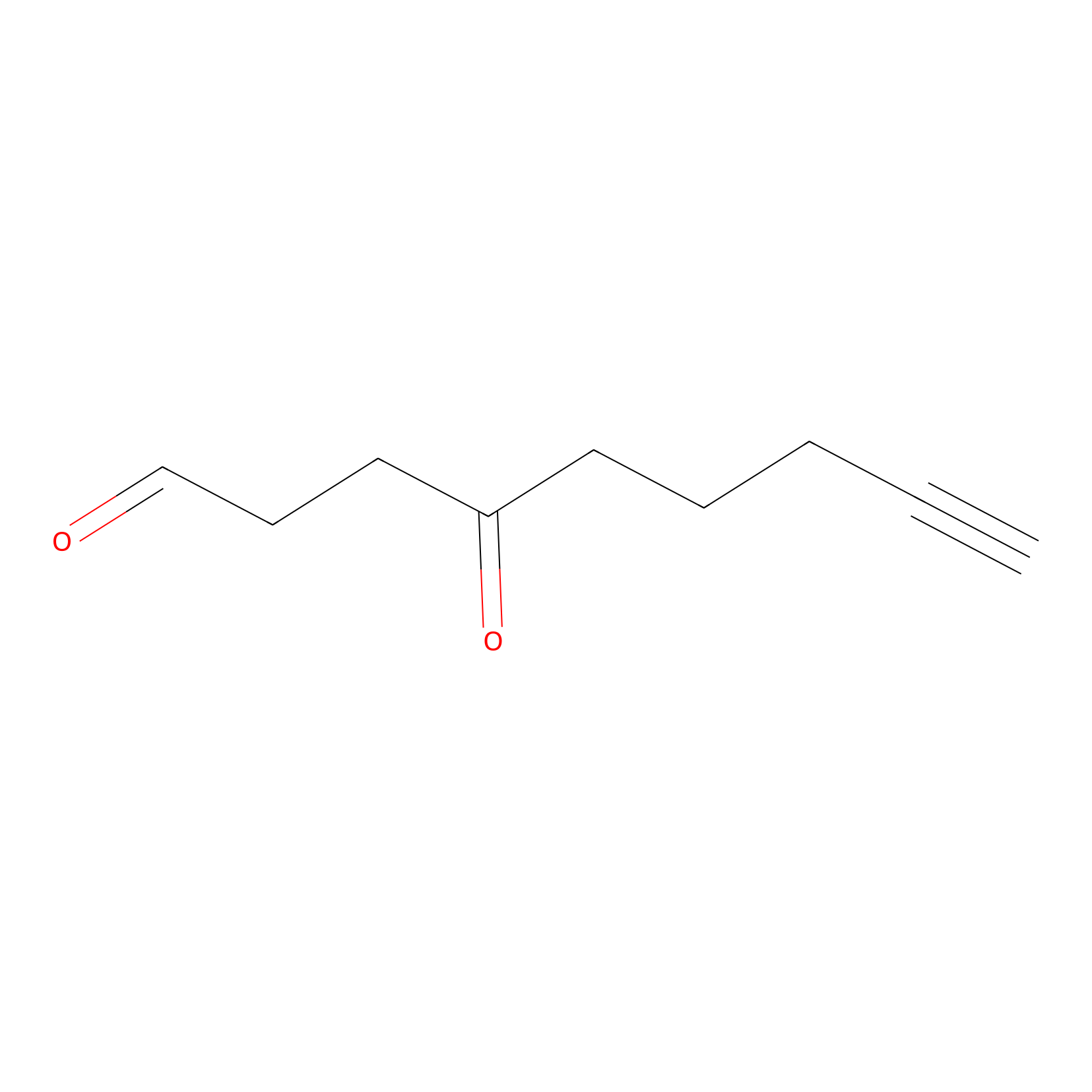 |
N.A. | LDD0273 | [3] | |
|
Probe 1 Probe Info |
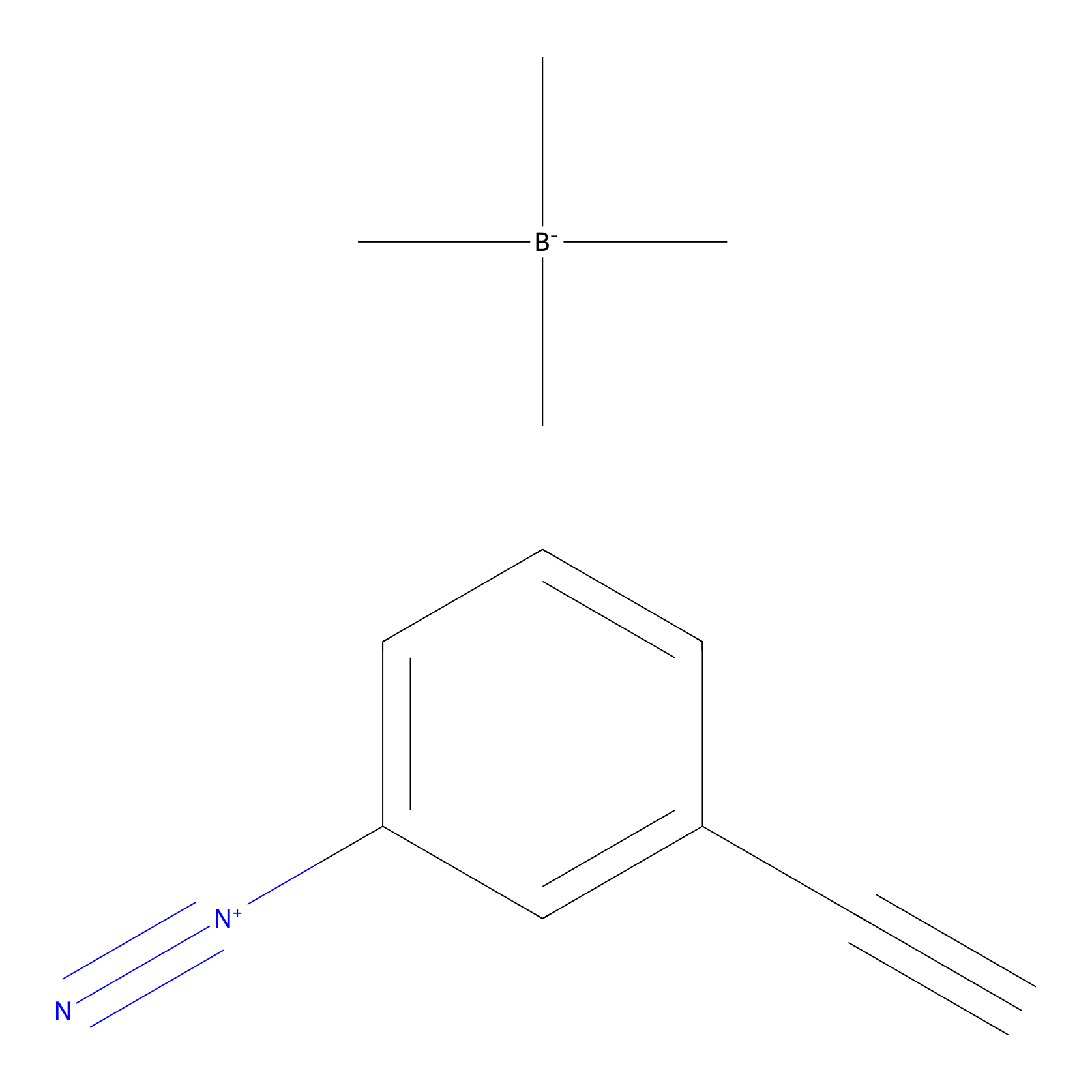 |
Y30(10.71); Y54(31.46); Y109(54.81); Y122(13.15) | LDD3495 | [4] | |
|
HHS-475 Probe Info |
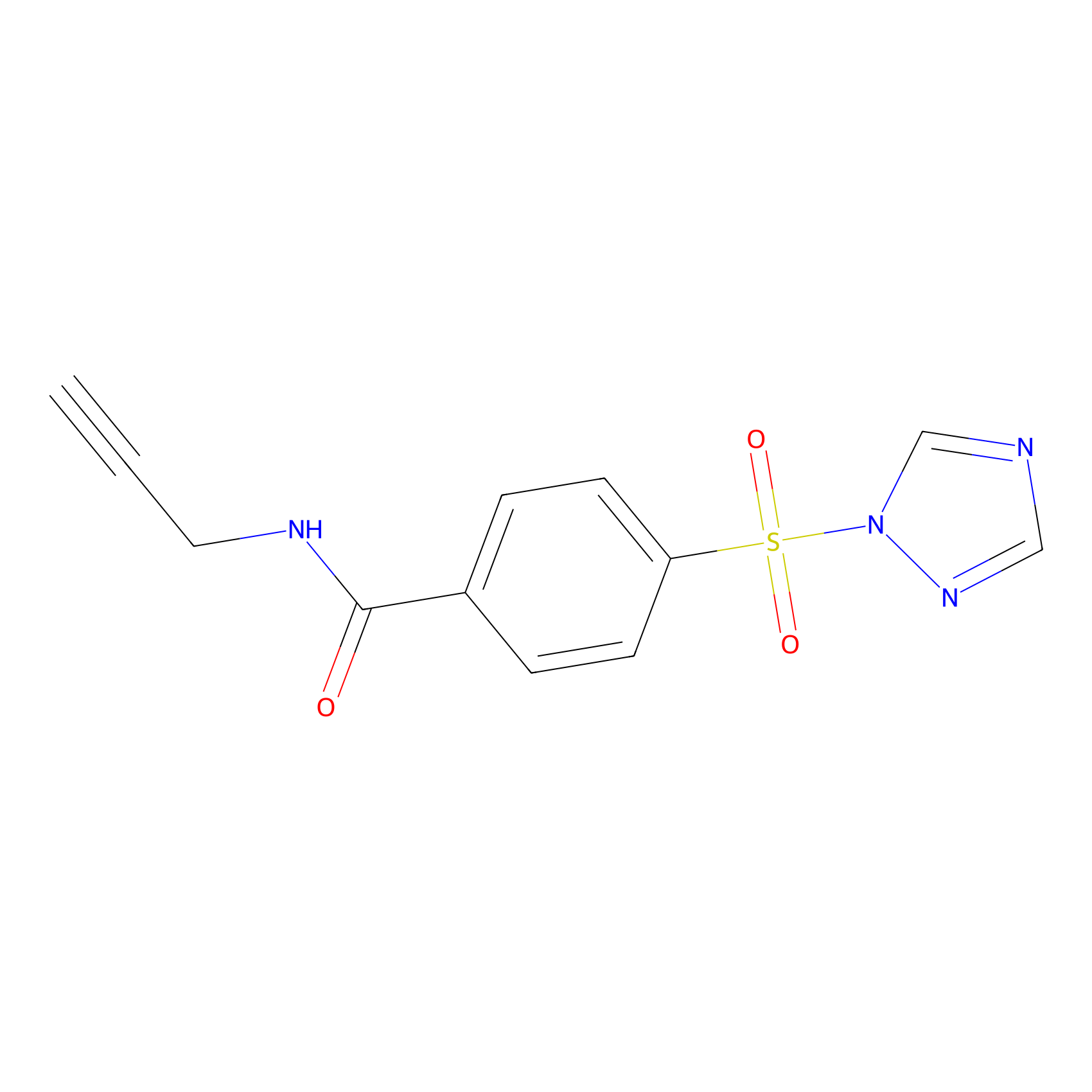 |
Y30(1.07) | LDD0264 | [5] | |
|
HHS-465 Probe Info |
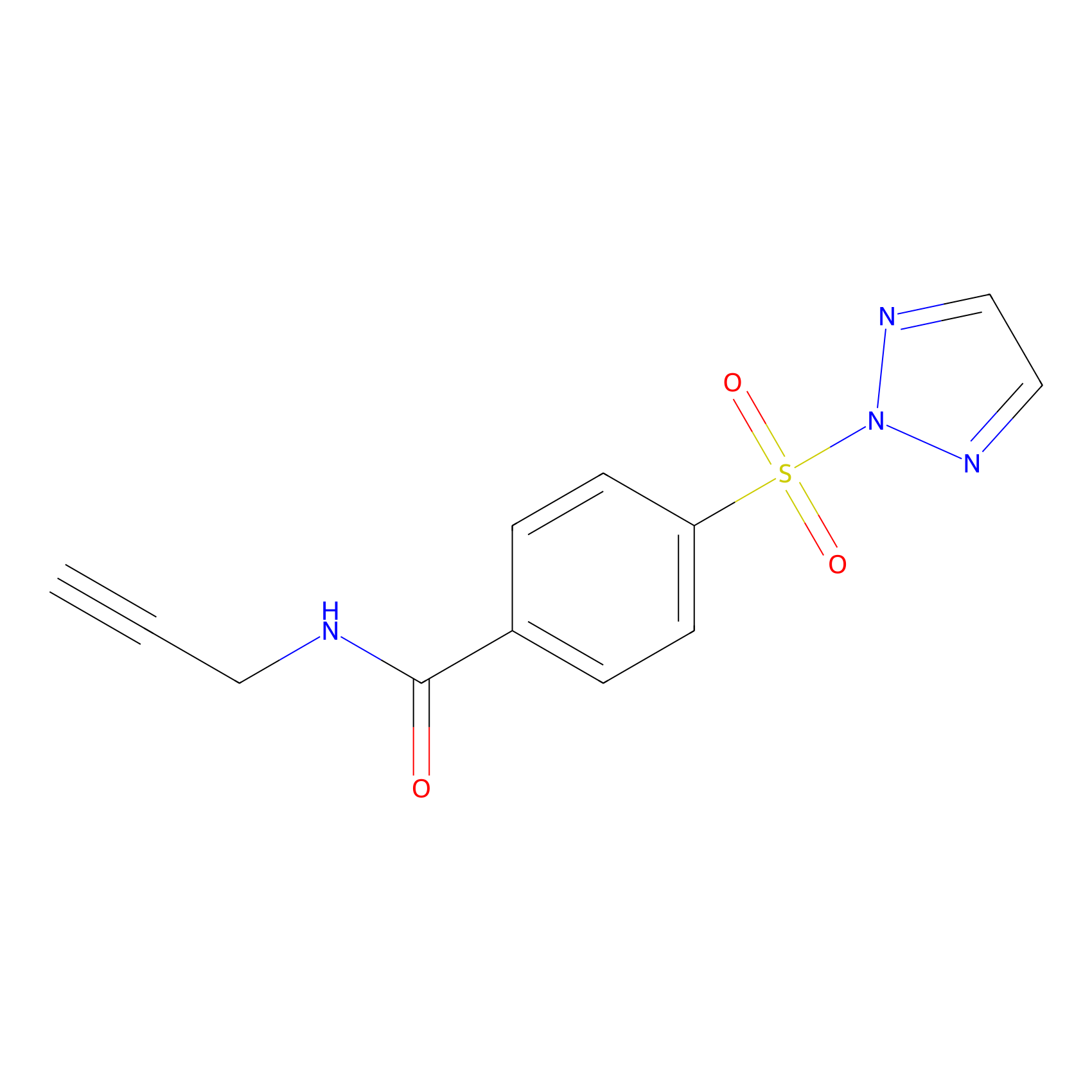 |
Y54(7.07) | LDD2237 | [6] | |
|
5E-2FA Probe Info |
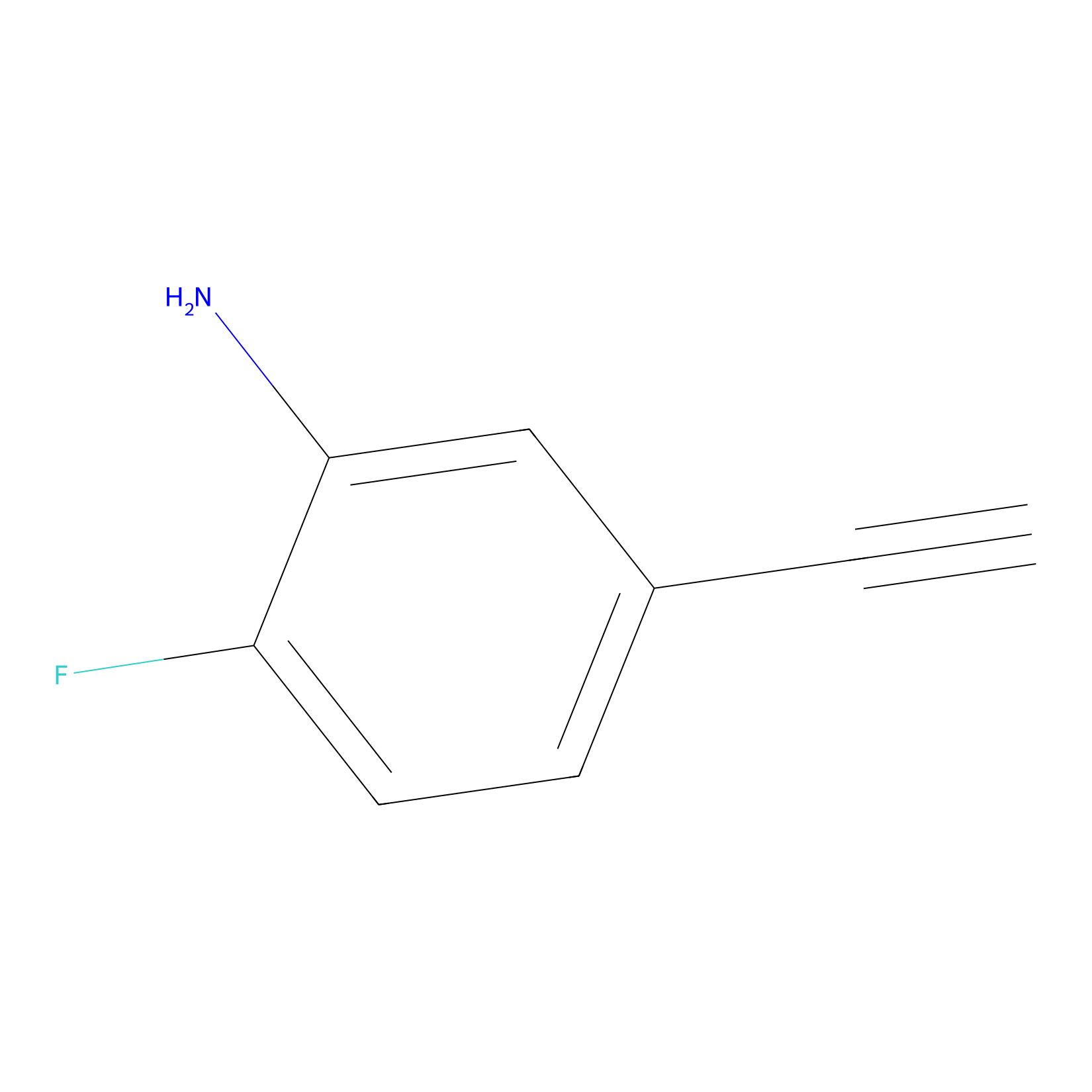 |
H29(0.00); H59(0.00) | LDD2235 | [7] | |
|
ATP probe Probe Info |
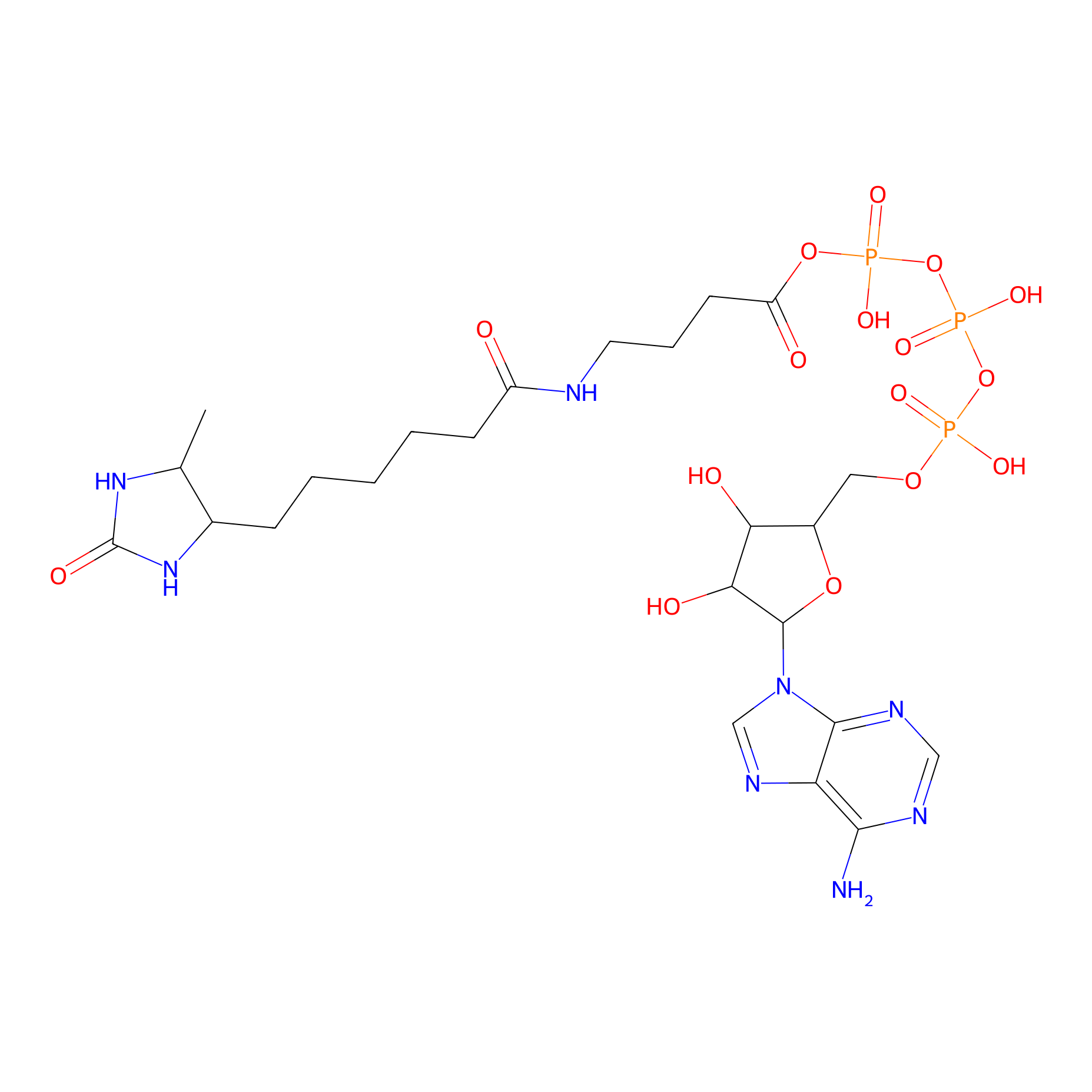 |
N.A. | LDD0199 | [8] | |
|
m-APA Probe Info |
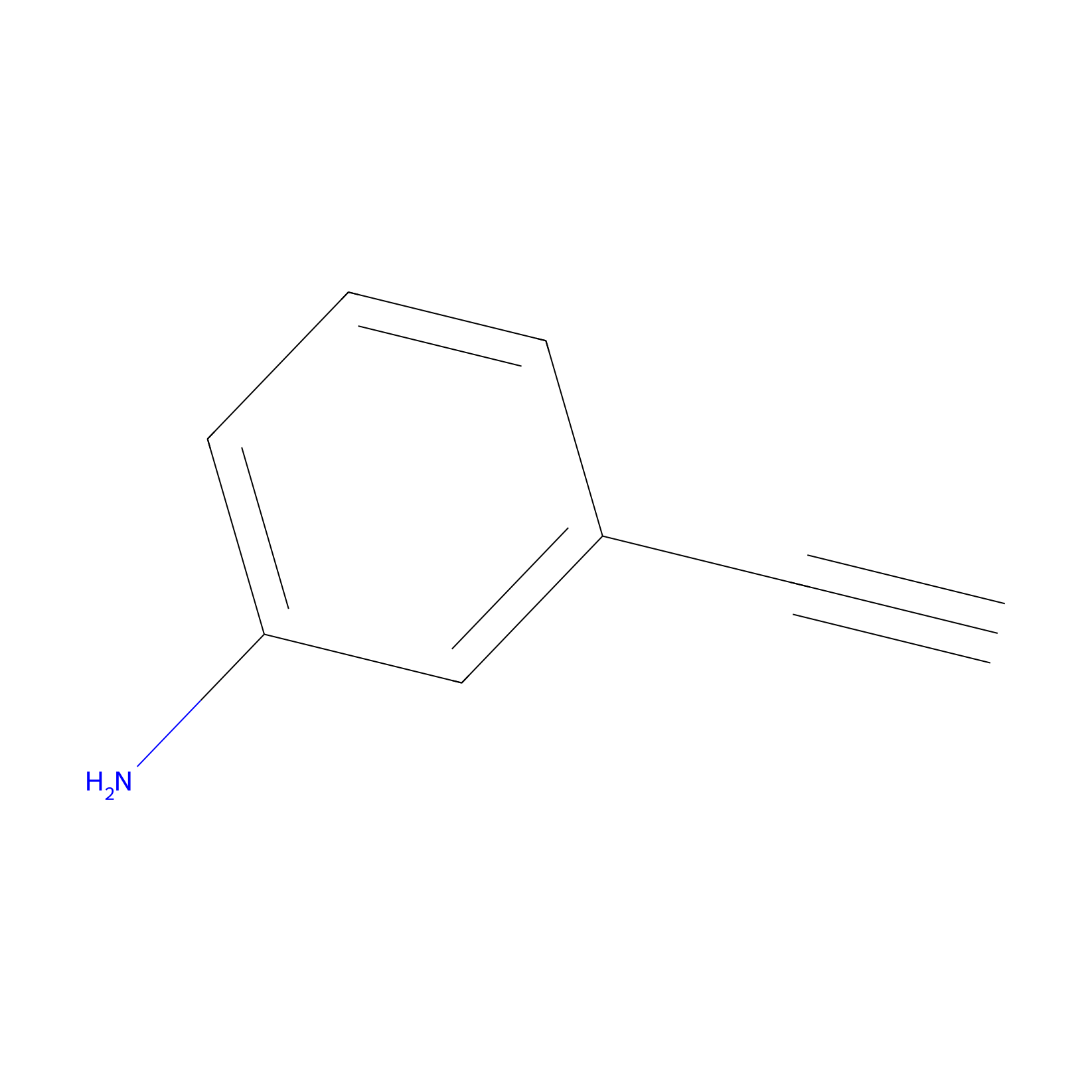 |
N.A. | LDD2231 | [7] | |
|
NHS Probe Info |
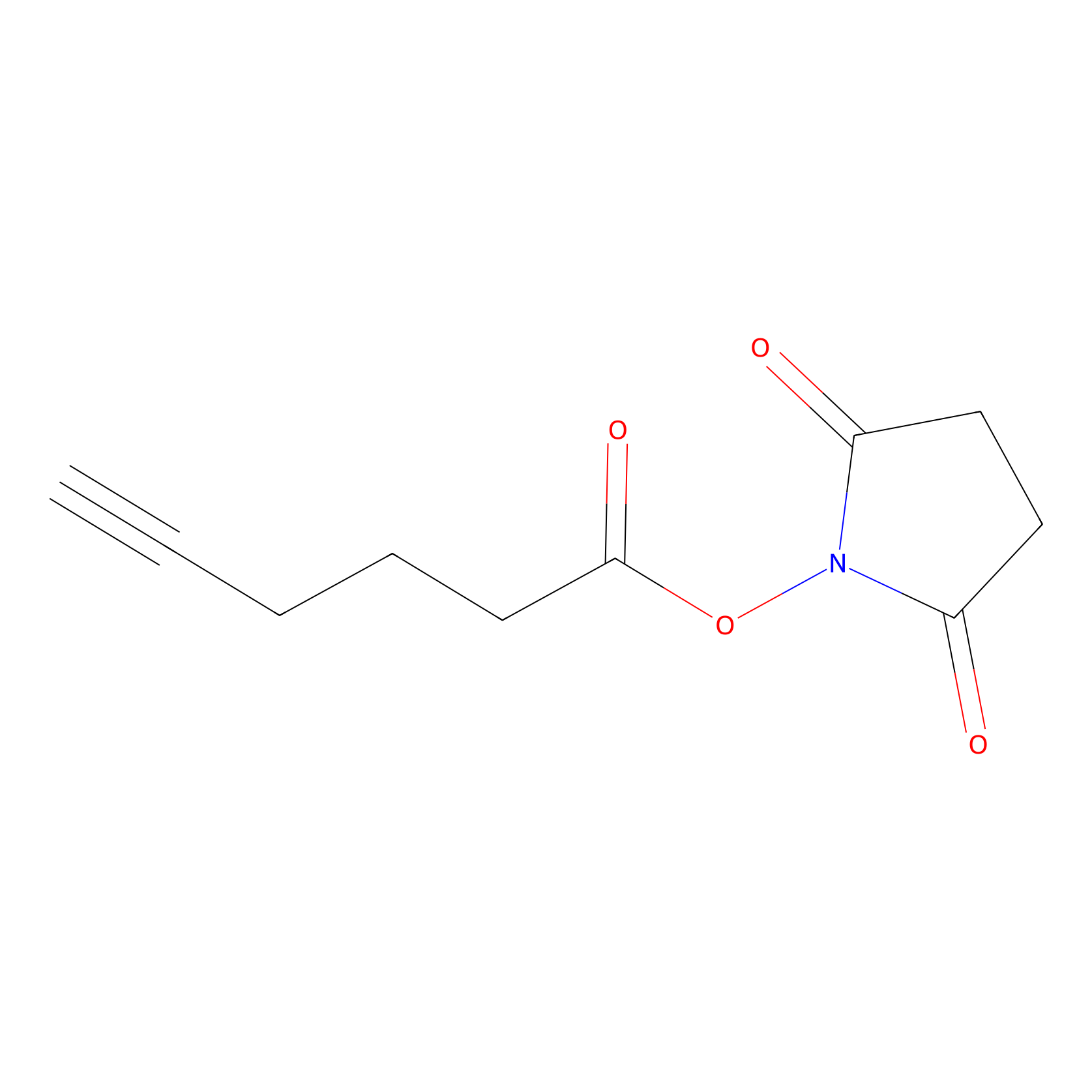 |
K241(0.00); K64(0.00) | LDD0010 | [9] | |
|
1c-yne Probe Info |
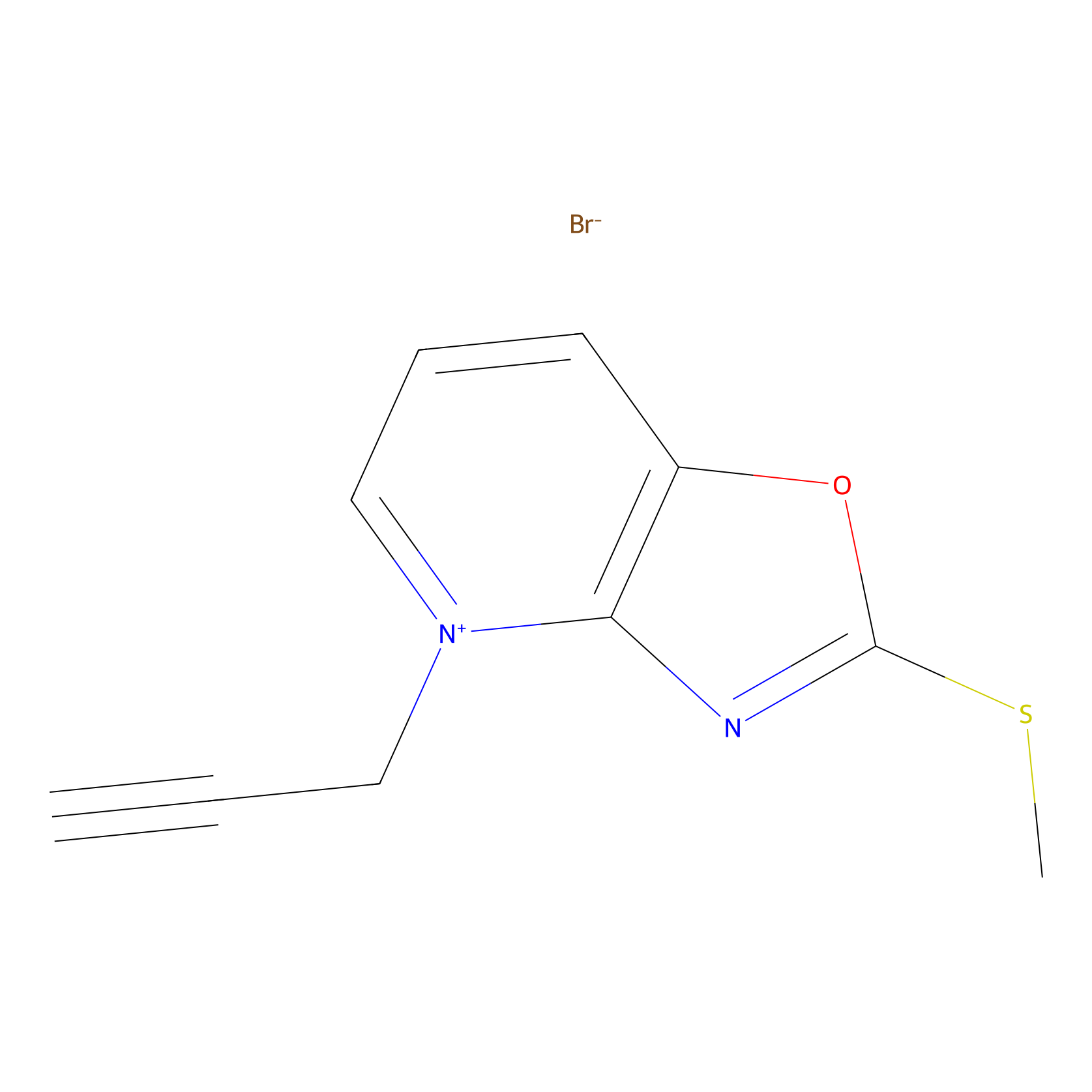 |
N.A. | LDD0228 | [10] | |
|
1d-yne Probe Info |
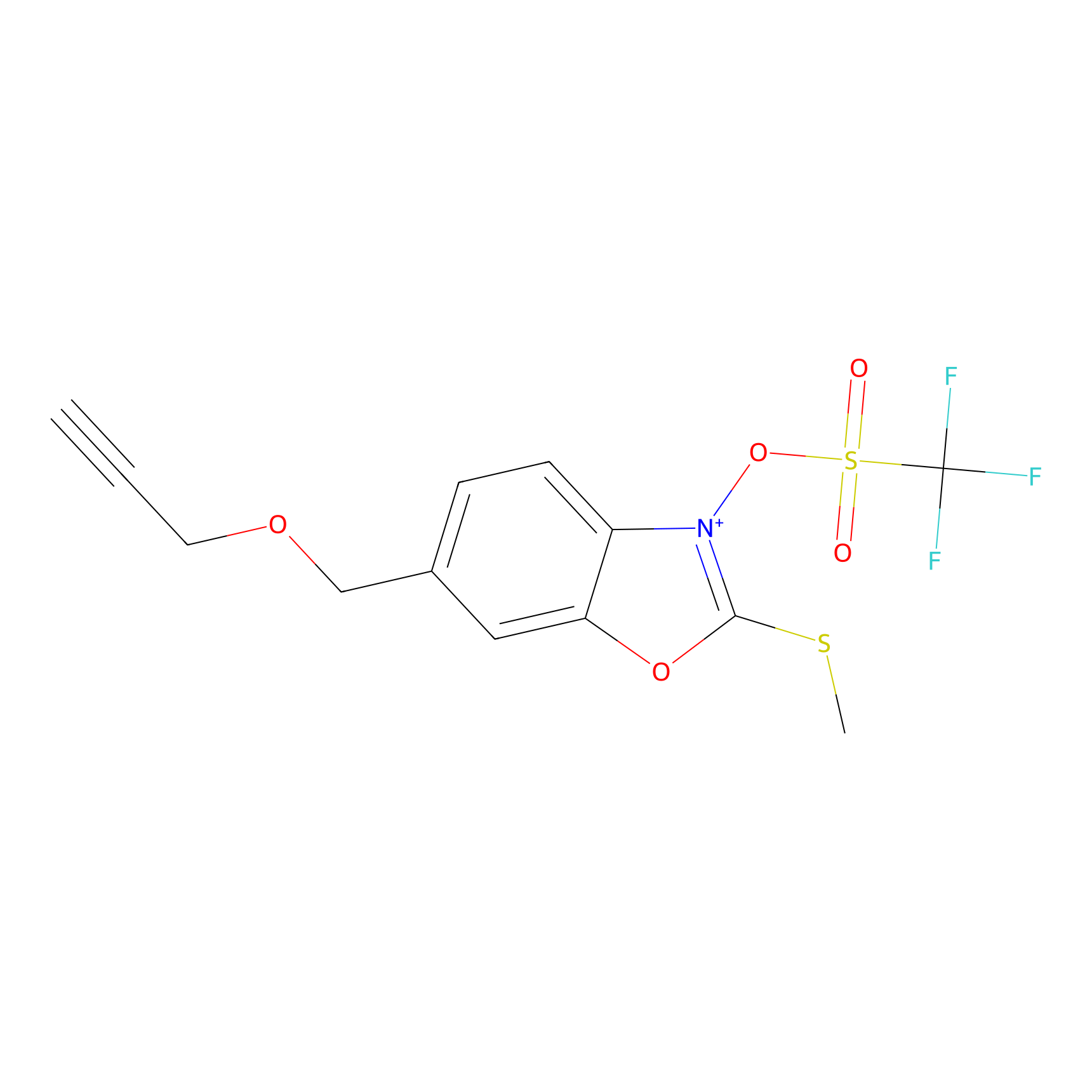 |
N.A. | LDD0357 | [10] | |
|
Acrolein Probe Info |
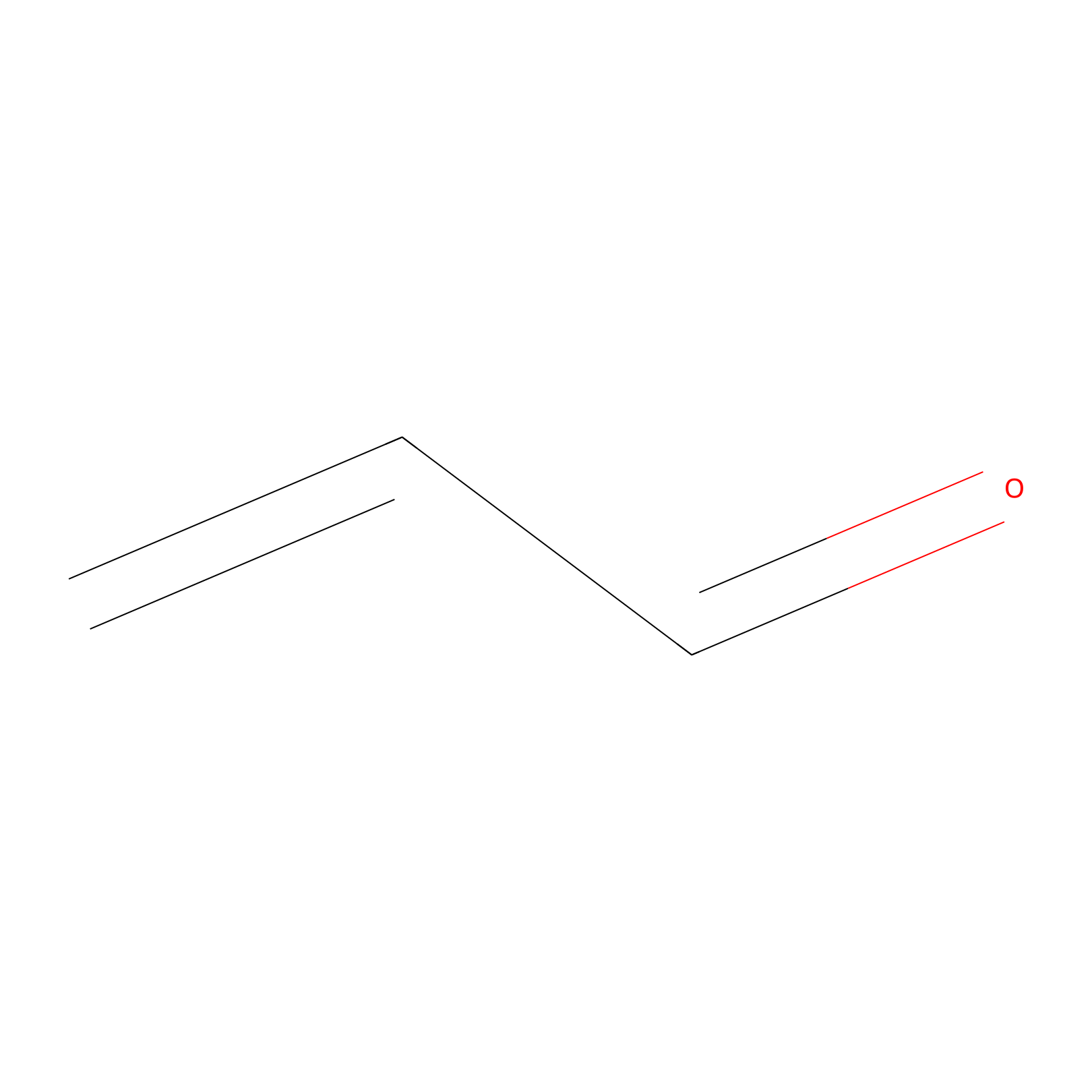 |
N.A. | LDD0217 | [11] | |
|
Crotonaldehyde Probe Info |
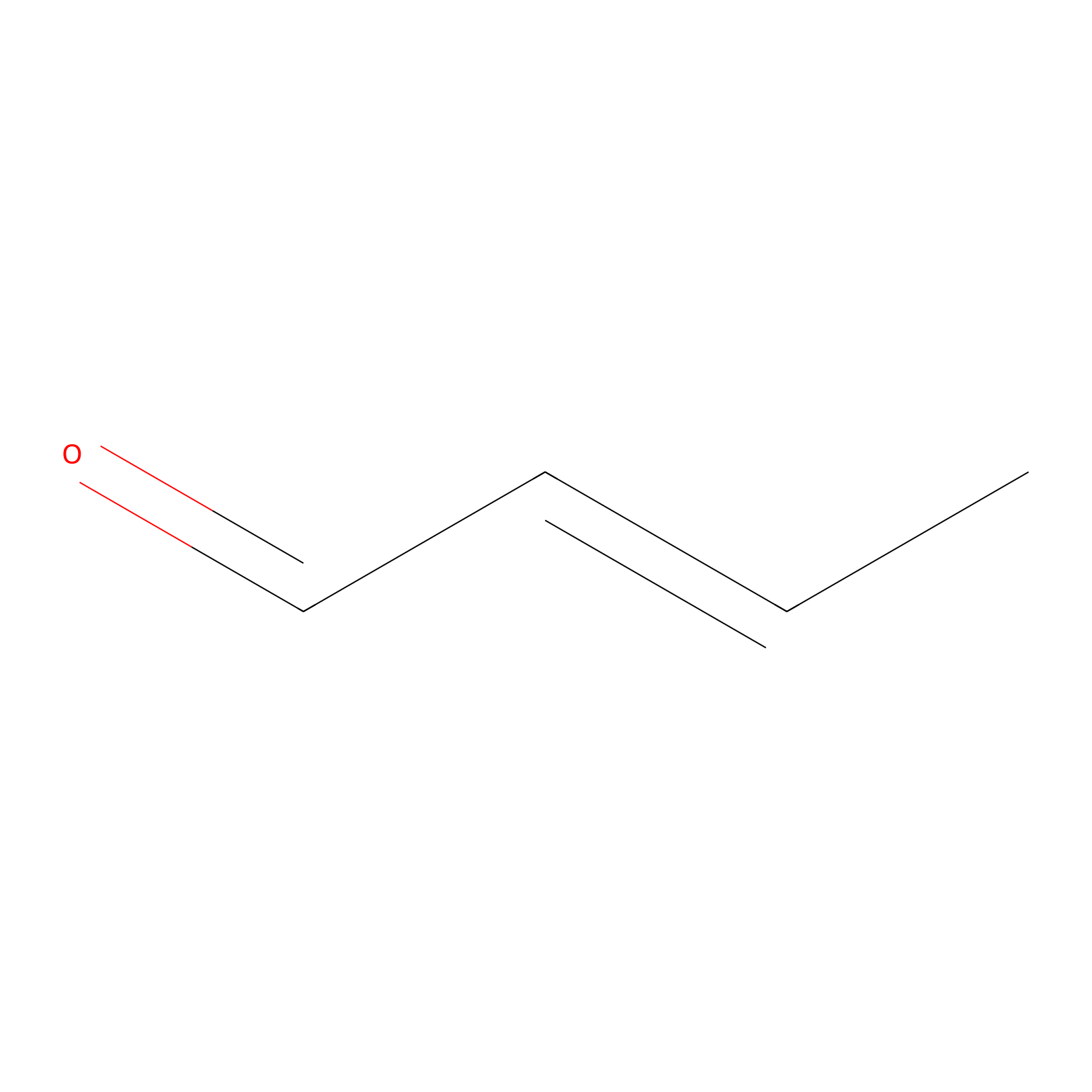 |
N.A. | LDD0219 | [11] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0108 | Chloroacetamide | HeLa | H96(0.00); H59(0.00) | LDD0222 | [11] |
| LDCM0116 | HHS-0101 | DM93 | Y30(1.07) | LDD0264 | [5] |
| LDCM0117 | HHS-0201 | DM93 | Y30(0.60) | LDD0265 | [5] |
| LDCM0118 | HHS-0301 | DM93 | Y30(0.76) | LDD0266 | [5] |
| LDCM0119 | HHS-0401 | DM93 | Y30(0.94) | LDD0267 | [5] |
| LDCM0120 | HHS-0701 | DM93 | Y30(0.76) | LDD0268 | [5] |
| LDCM0107 | IAA | HeLa | H96(0.00); H59(0.00) | LDD0221 | [11] |
| LDCM0109 | NEM | HeLa | H59(0.00); H308(0.00); H96(0.00); H29(0.00) | LDD0223 | [11] |
The Interaction Atlas With This Target
The Protein(s) Related To This Target
Enzyme
| Protein name | Family | Uniprot ID | |||
|---|---|---|---|---|---|
| E3 ubiquitin-protein ligase CHIP (STUB1) | . | Q9UNE7 | |||
Other
References