Details of the Target
General Information of Target
| Target ID | LDTP20002 | |||||
|---|---|---|---|---|---|---|
| Target Name | Transmembrane protein 160 (TMEM160) | |||||
| Gene Name | TMEM160 | |||||
| Gene ID | 54958 | |||||
| Synonyms |
Transmembrane protein 160 |
|||||
| 3D Structure | ||||||
| Sequence |
MEPNSLRTKVPAFLSDLGKATLRGIRKCPRCGTYNGTRGLSCKNKTCGTIFRYGARKQPS
VEAVKIITGSDLQVYSVRQRDRGPDYRCFVELGVSETTIQTVDGTIITQLSSGRCYVPSC LKAATQGVVENQCQHIKLAVNCQAEATPLTLKSSVLNAMQASPETKQTIWQLATEPTGPL VQRITKNILVVKCKASQKHSLGYLHTSFVQKVSGKSLPERRFFCSCQTLKSHKSNASKDE TAQRCIHFFACICAFASDETLAQEFSDFLNFDSSGLKEIIVPQLGCHSESTVSACESTAS KSKKRRKDEVSGAQMNSSLLPQDAVSSNLRKSGLKKPVVASSLKRQACGQLLDEAQVTLS FQDWLASVTERIHQTMHYQFDGKPEPLVFHIPQSFFDALQQRISIGSAKKRLPNSTTAFV RKDALPLGTFSKYTWHITNILQVKQILDTPEMPLEITRSFIQNRDGTYELFKCPKVEVES IAETYGRIEKQPVLRPLELKTFLKVGNTSPDQKEPTPFIIEWIPDILPQSKIGELRIKFE YGHHRNGHVAEYQDQRPPLDQPLELAPLTTITFP |
|||||
| Target Bioclass |
Transporter and channel
|
|||||
| Family |
TMEM160 family
|
|||||
| Subcellular location |
Mitochondrion inner membrane
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Probe(s) Labeling This Target
ABPP Probe
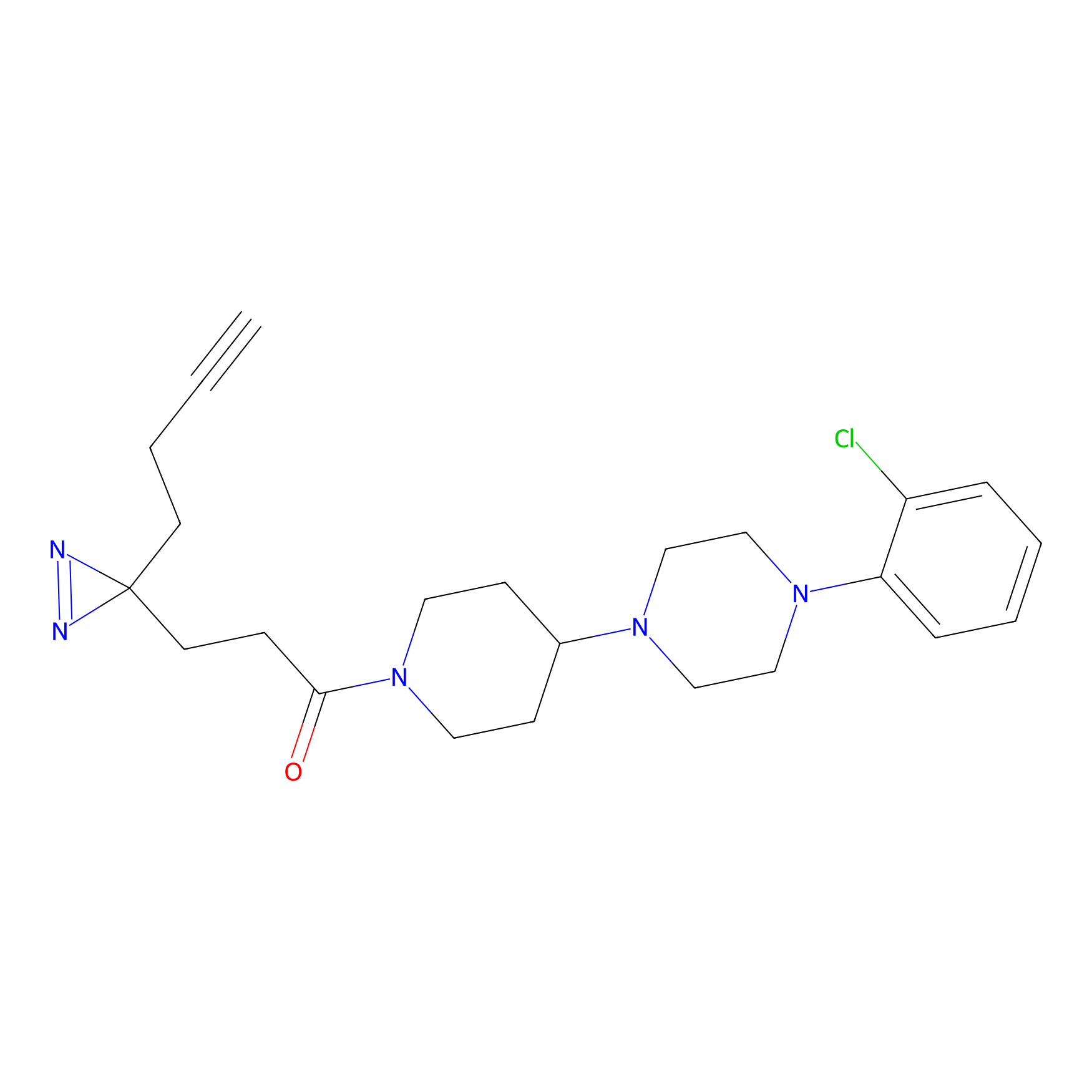
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
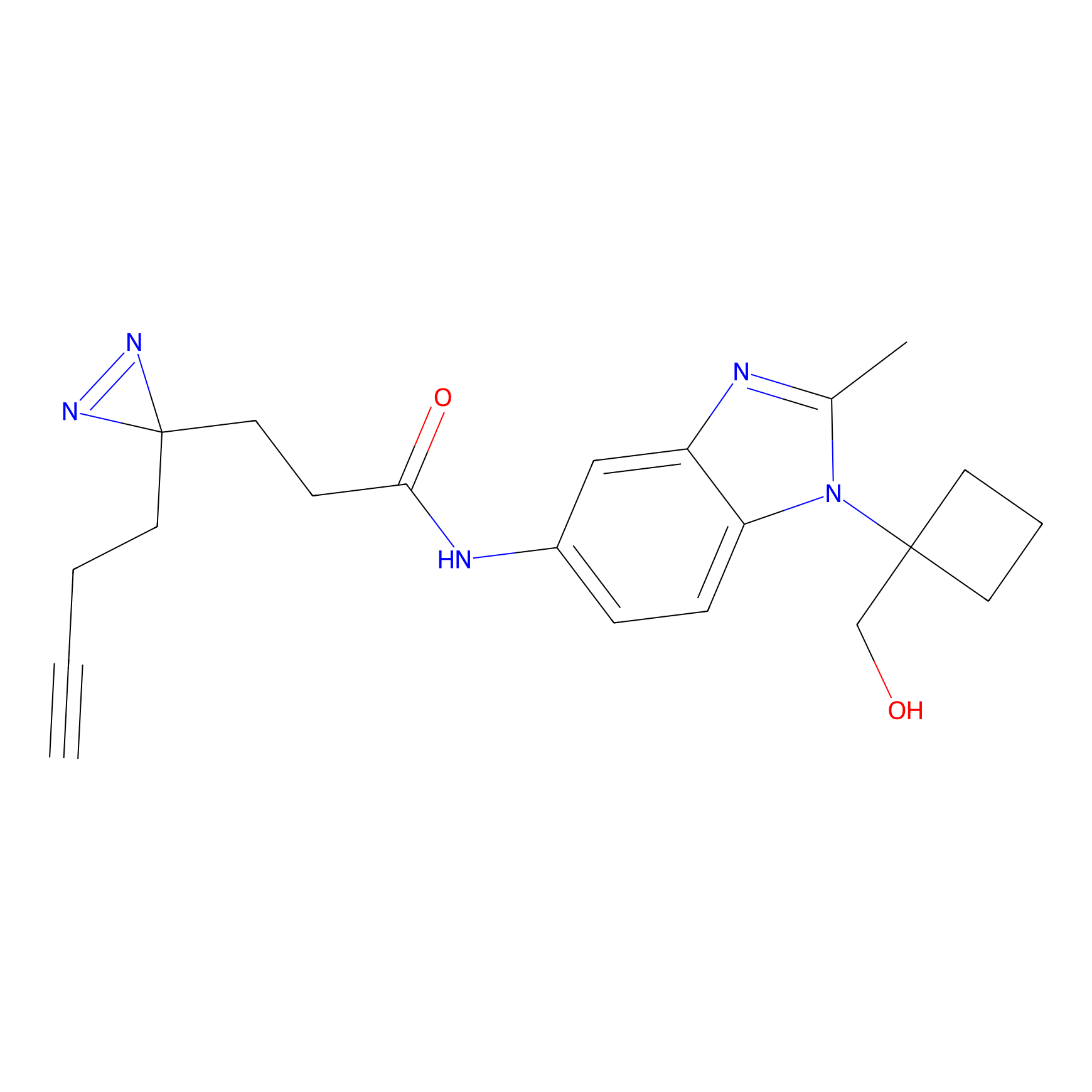
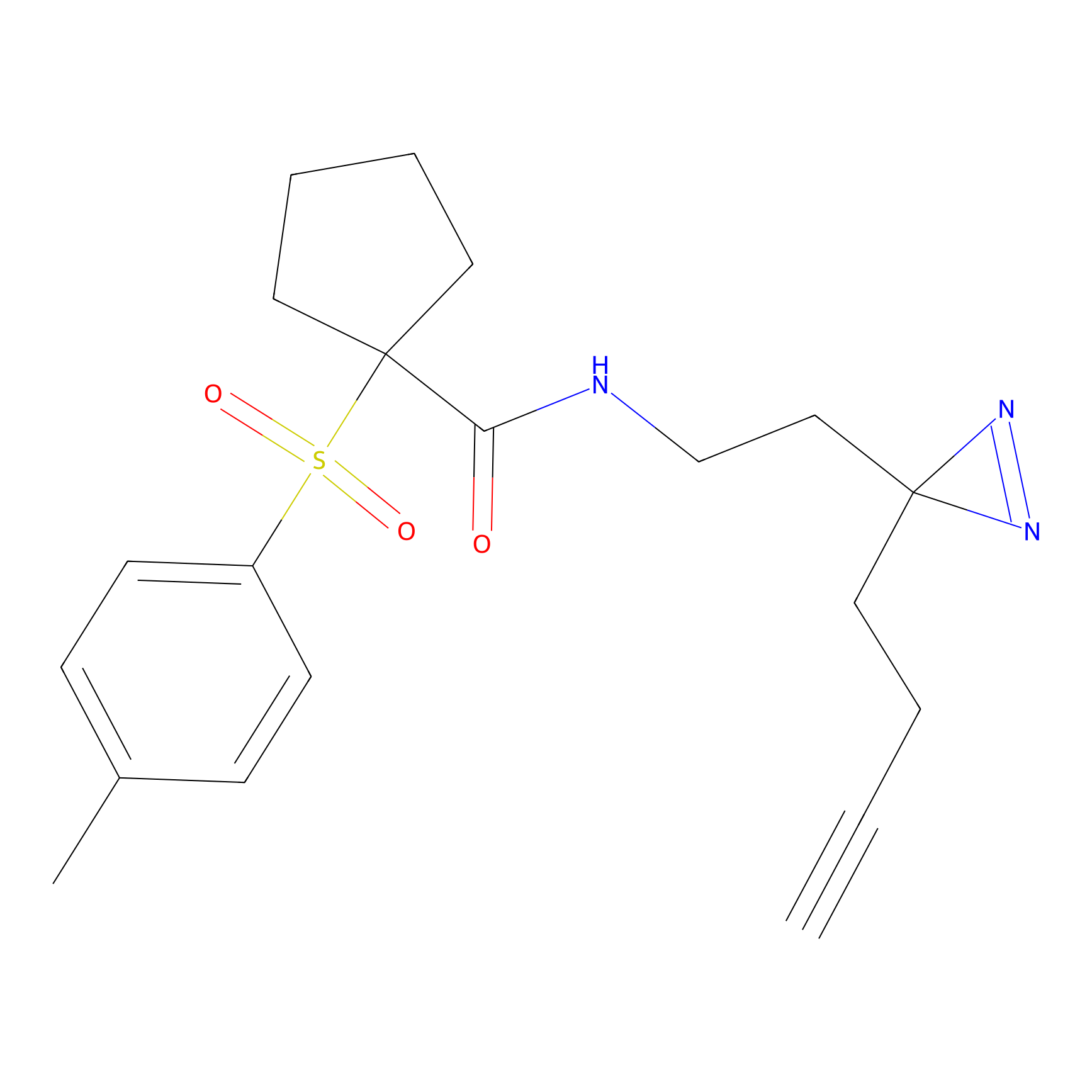
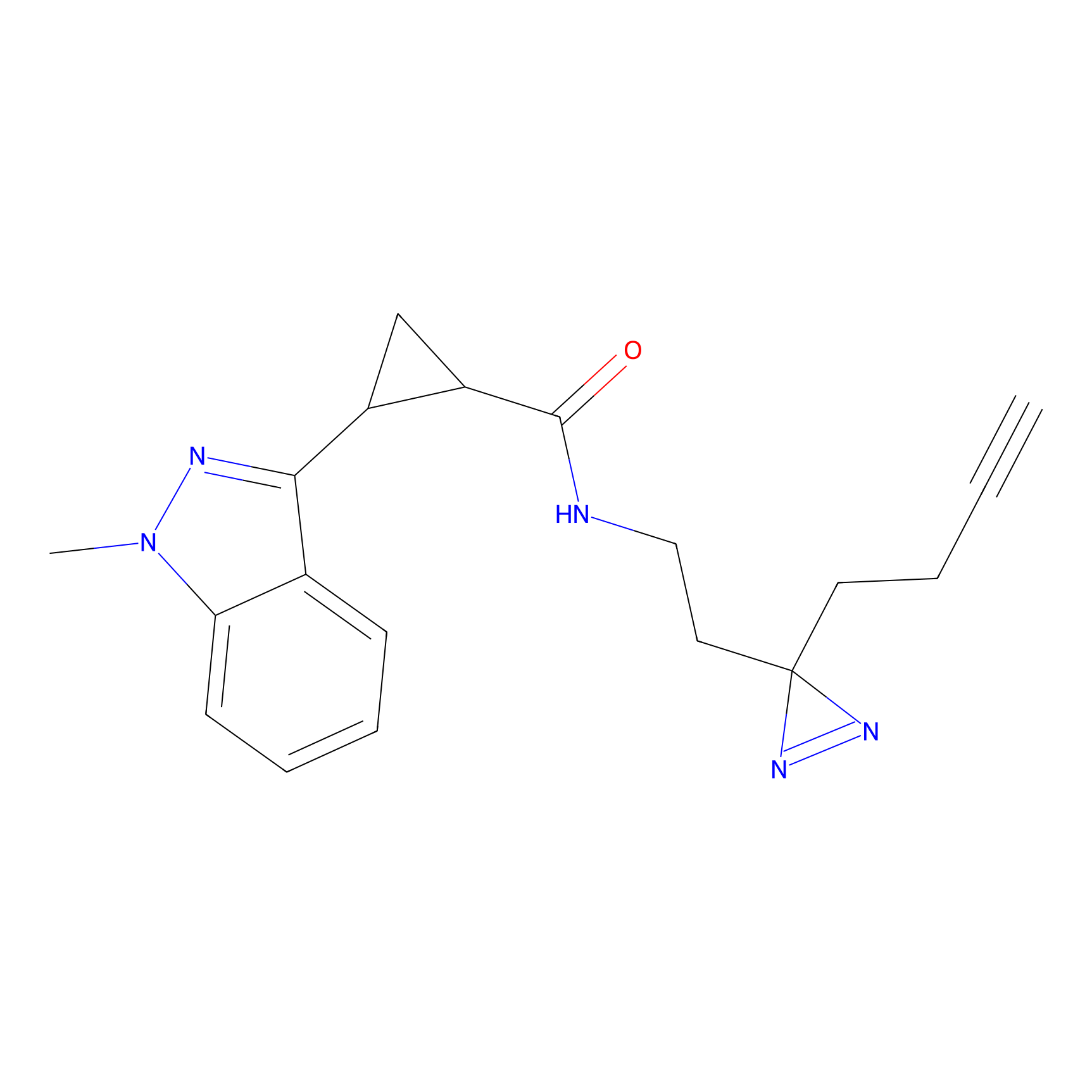
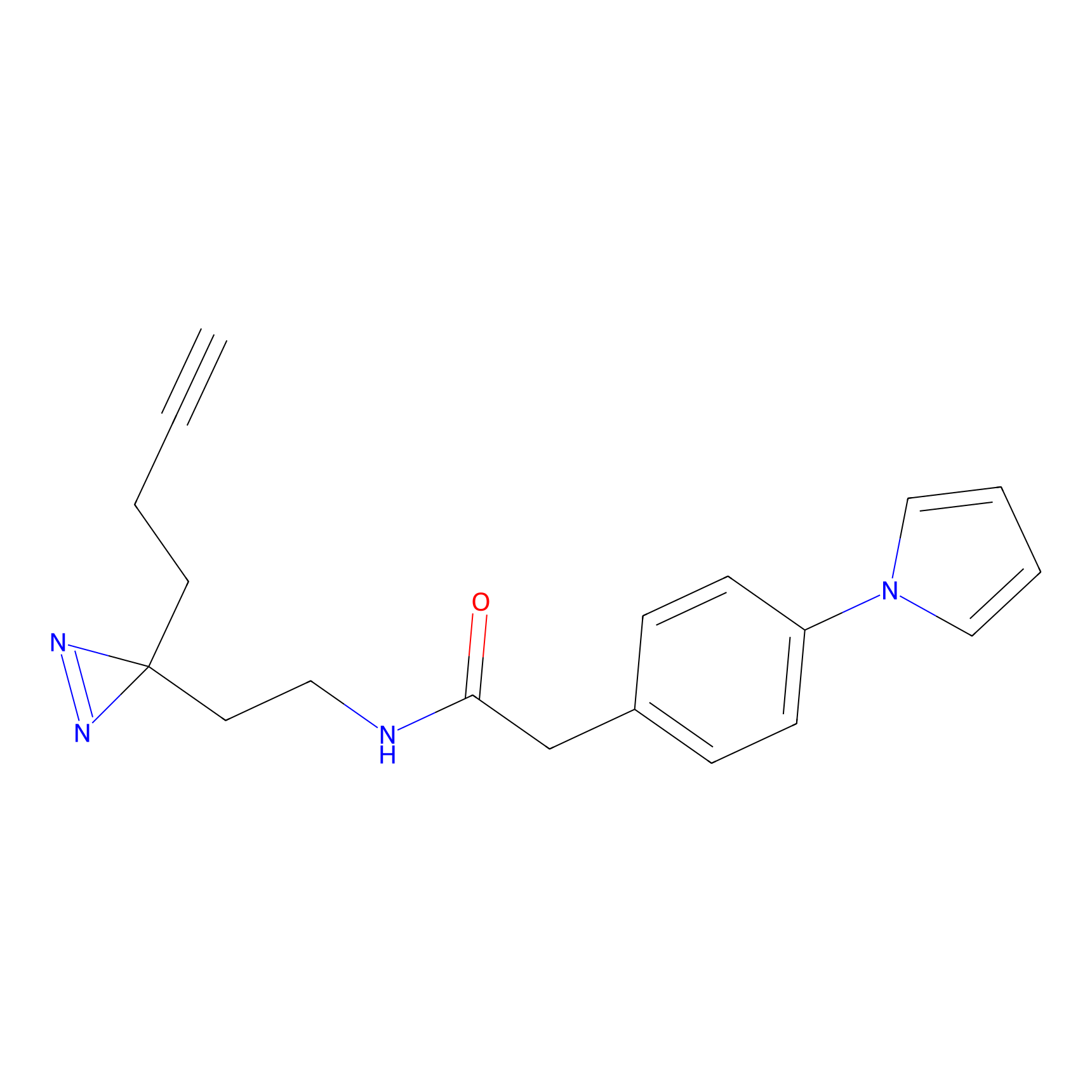
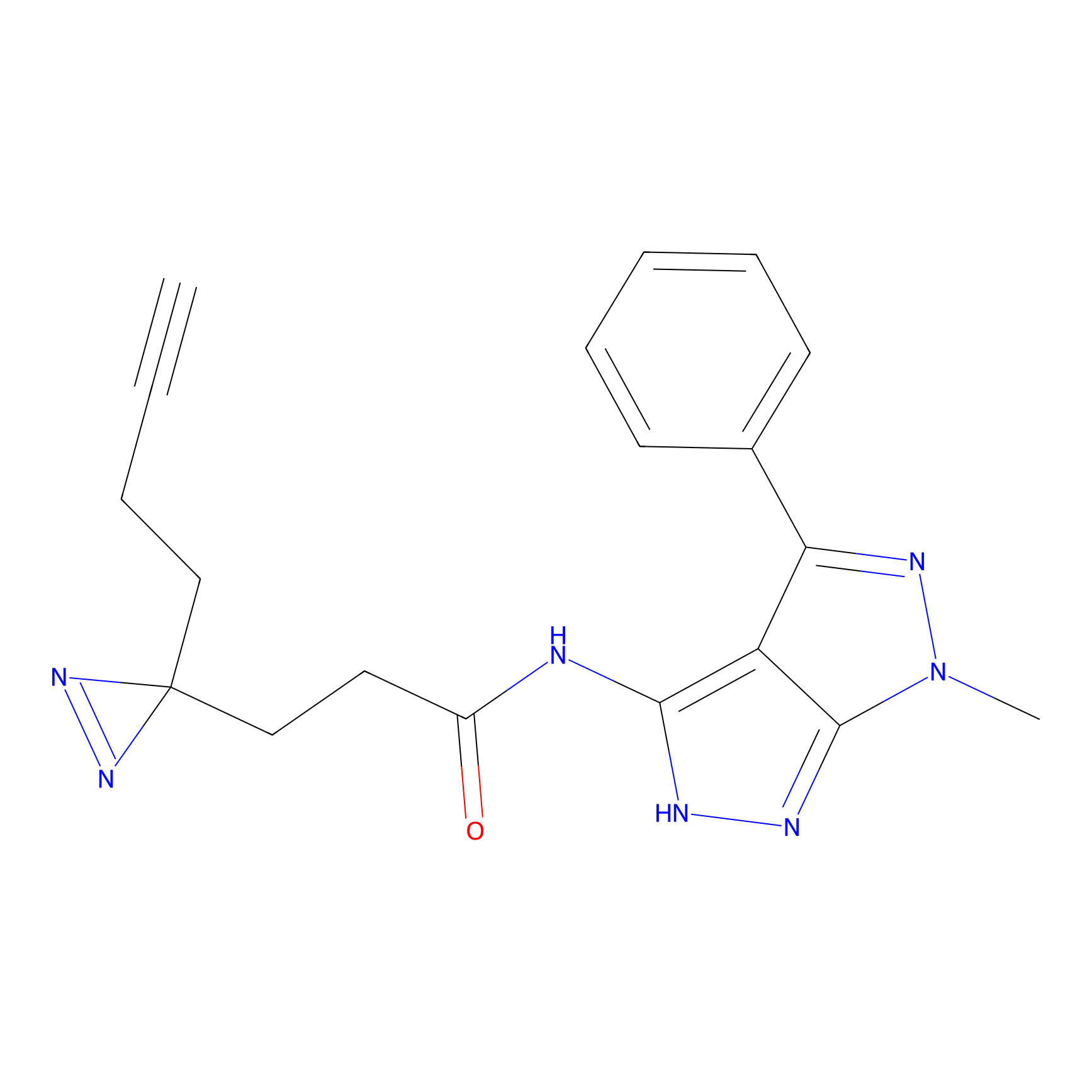
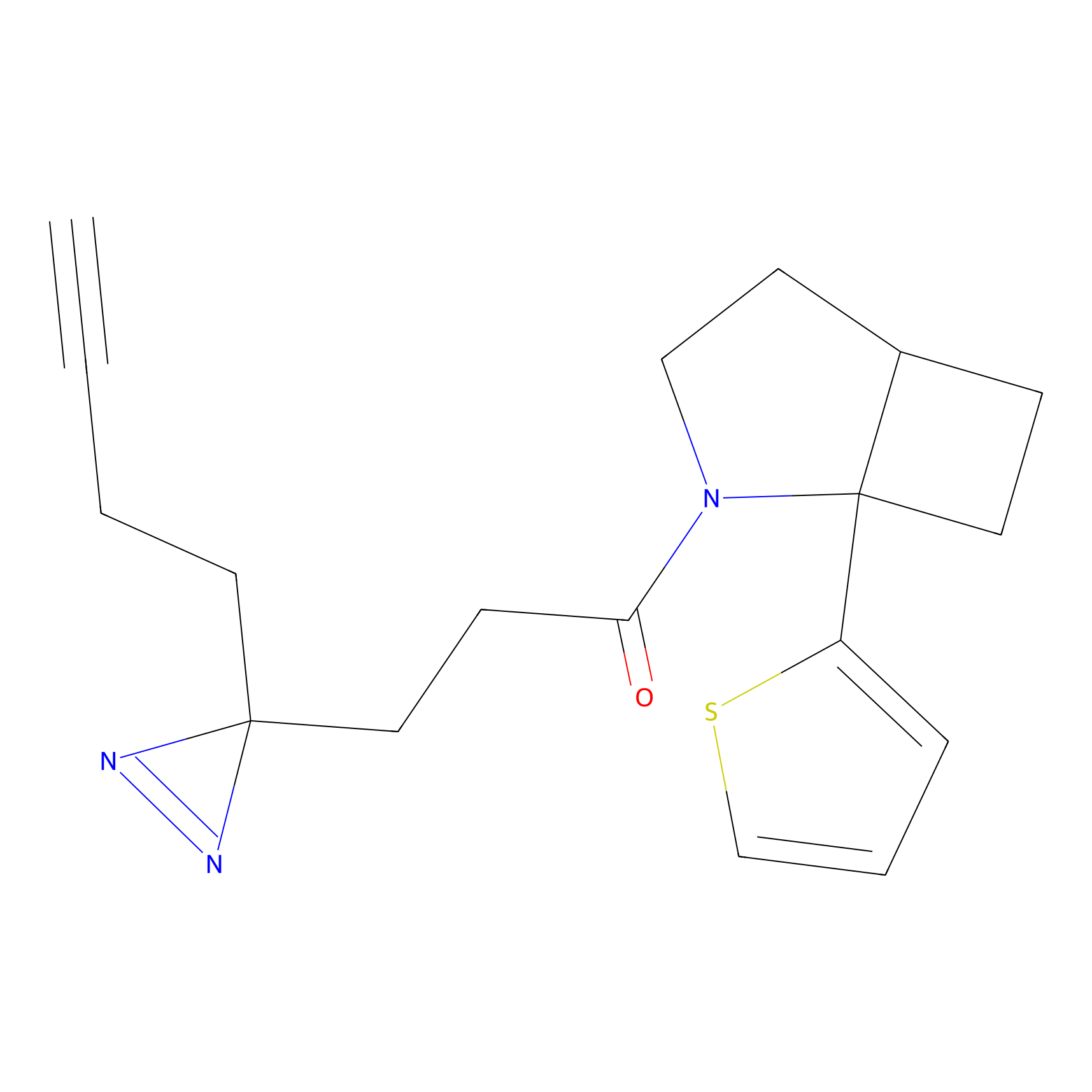
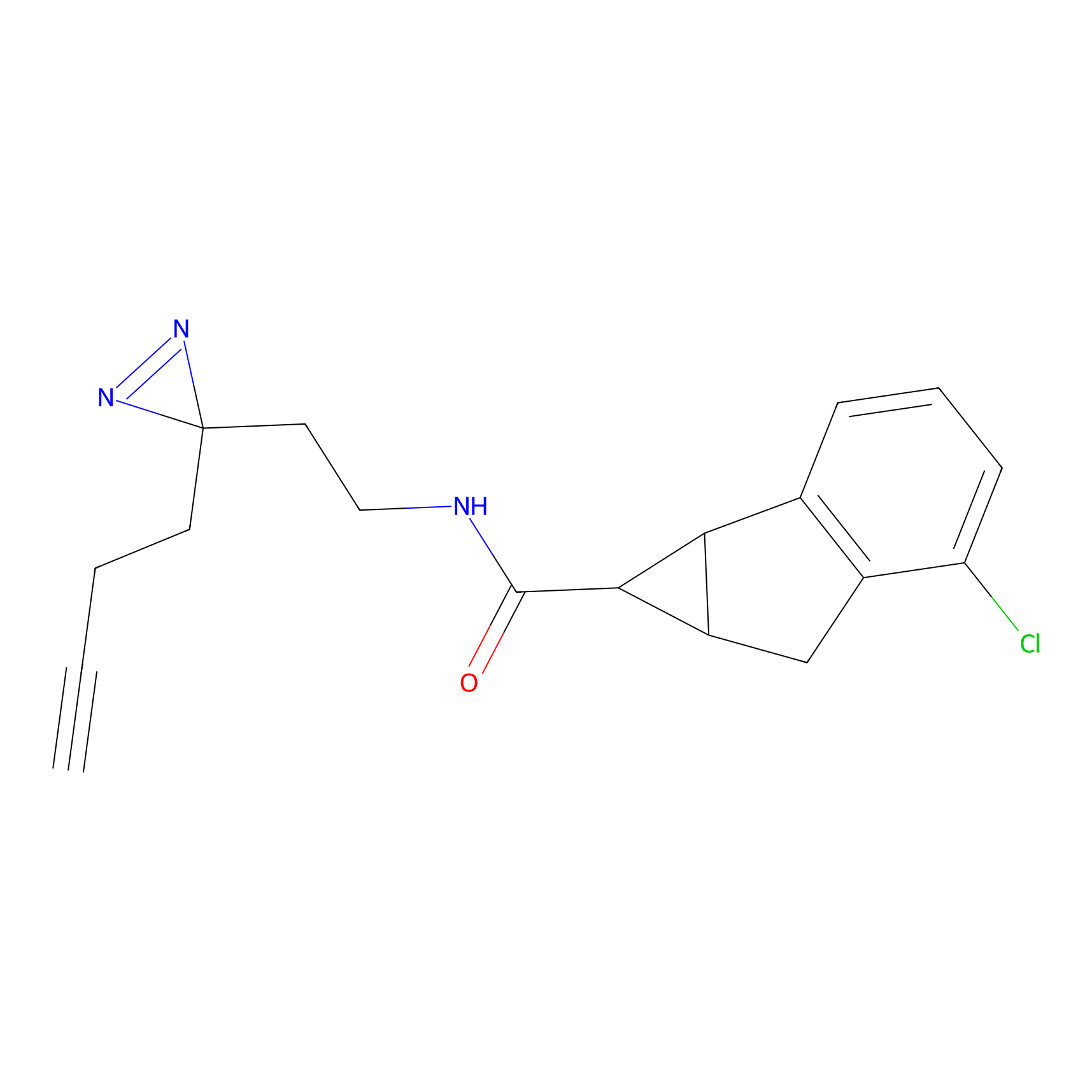
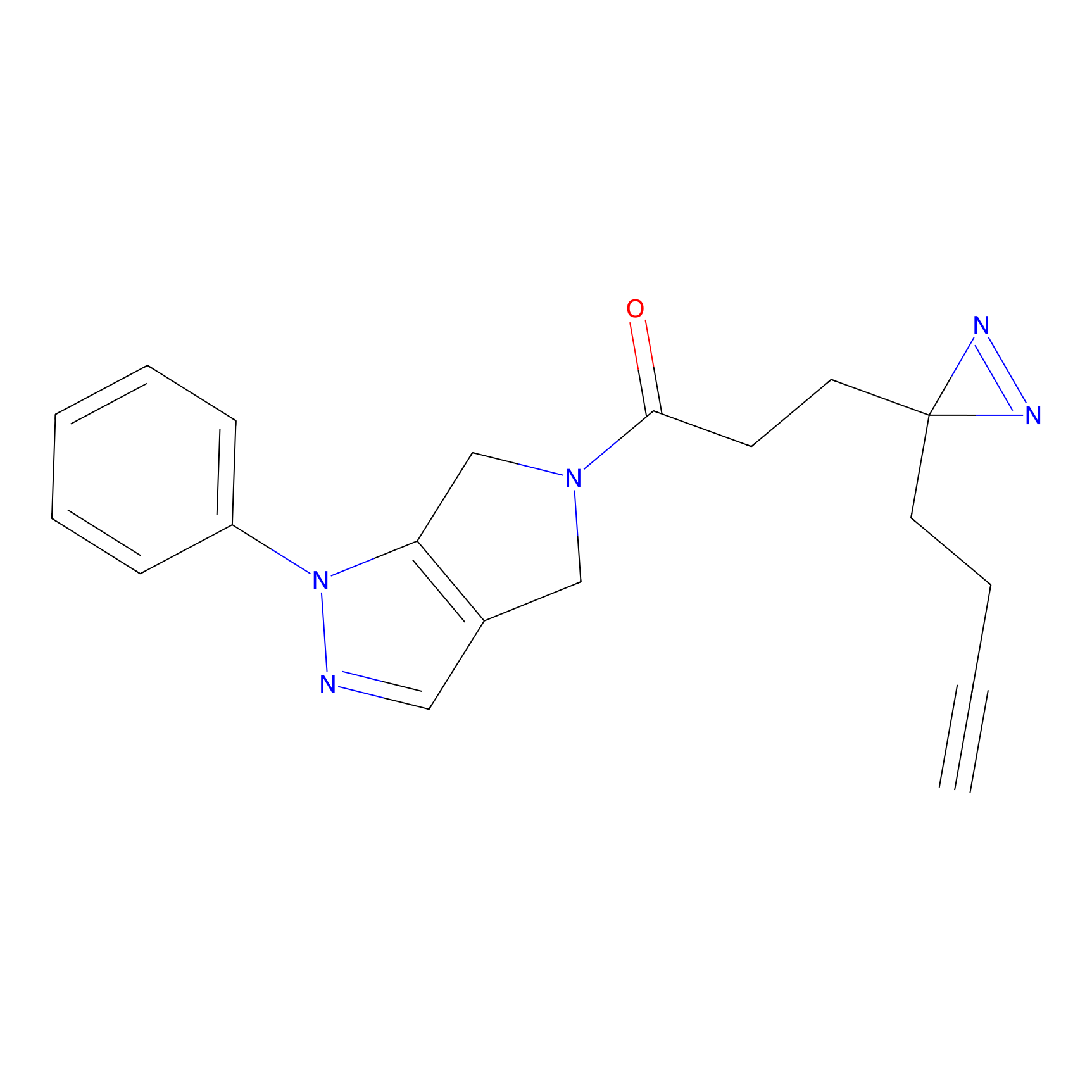
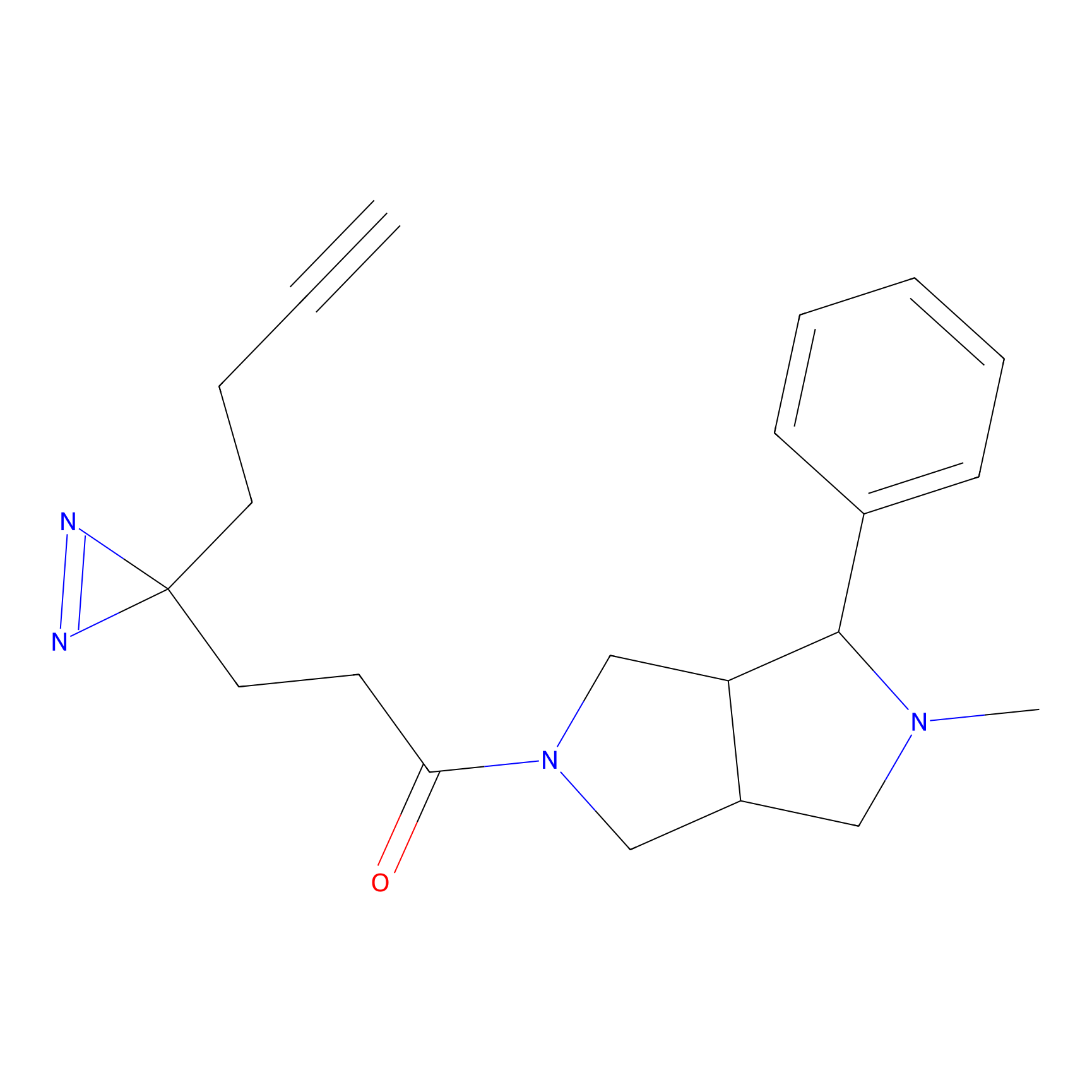
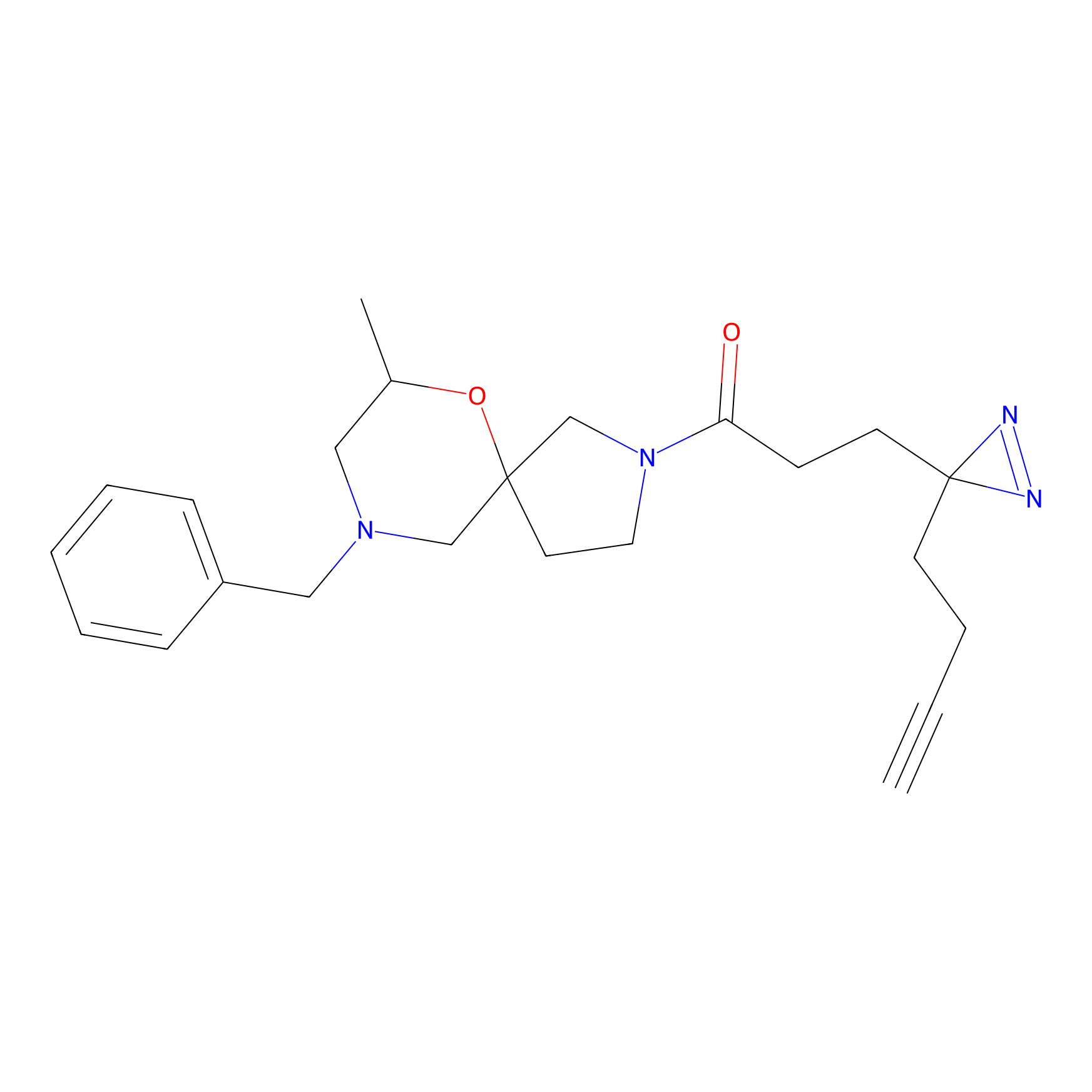
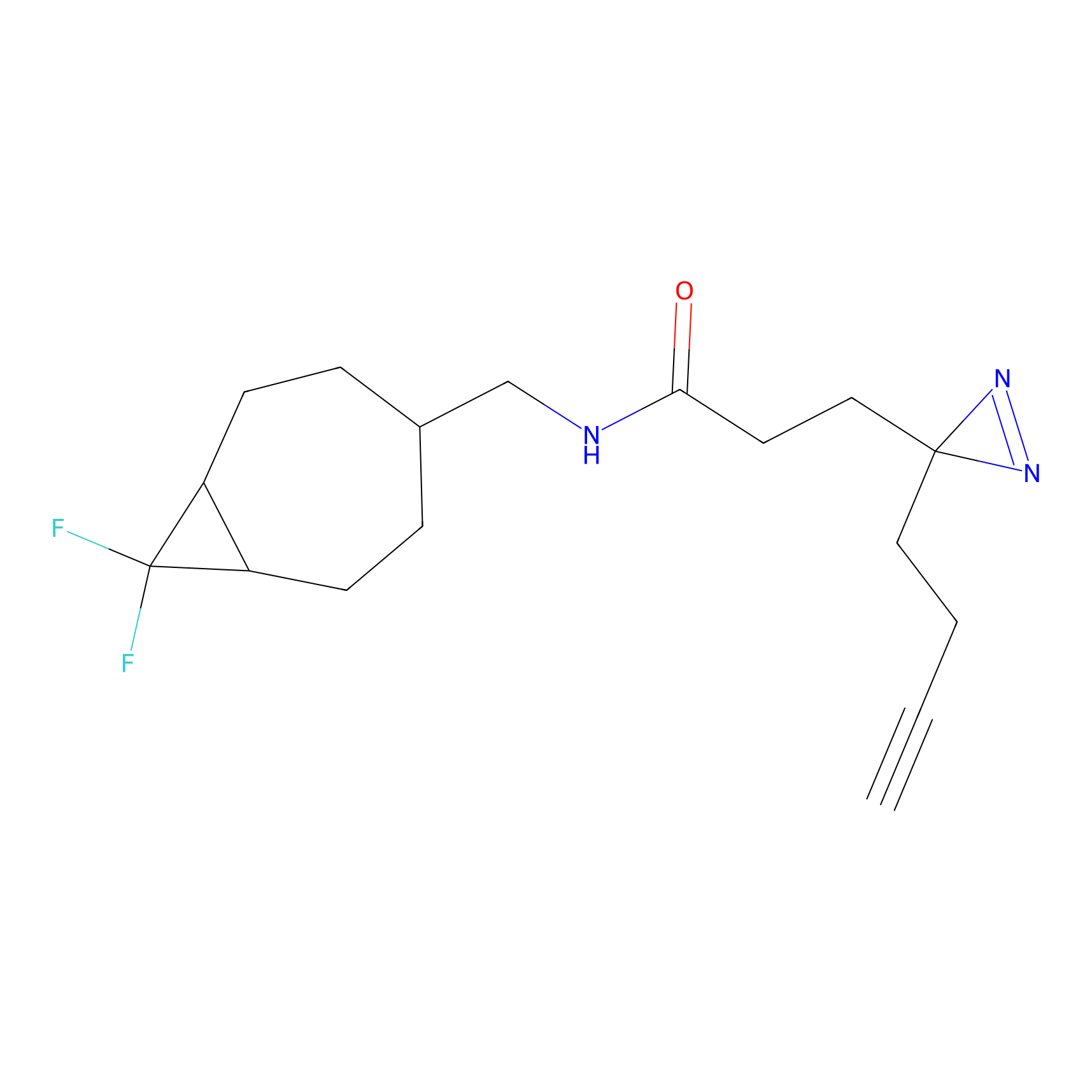
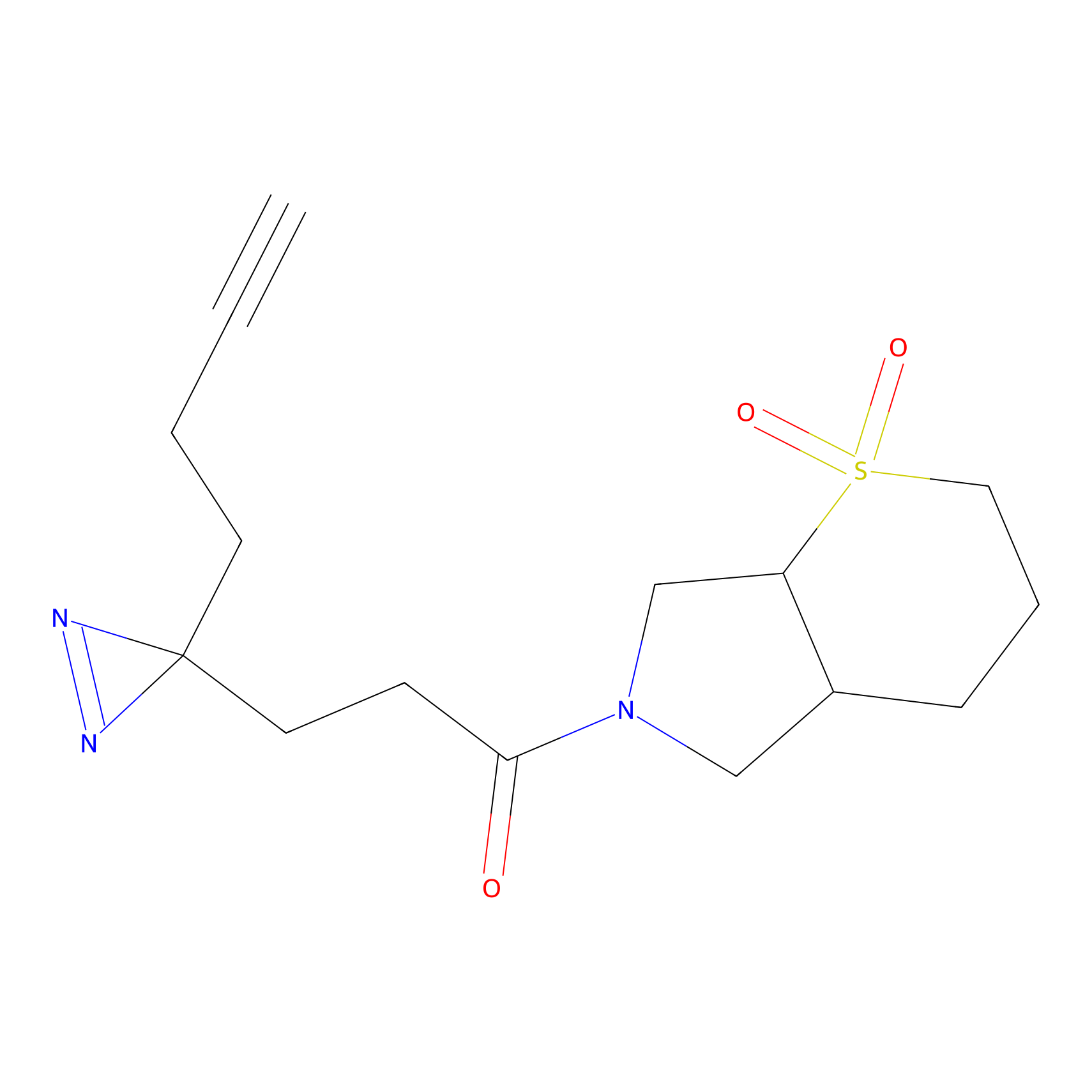
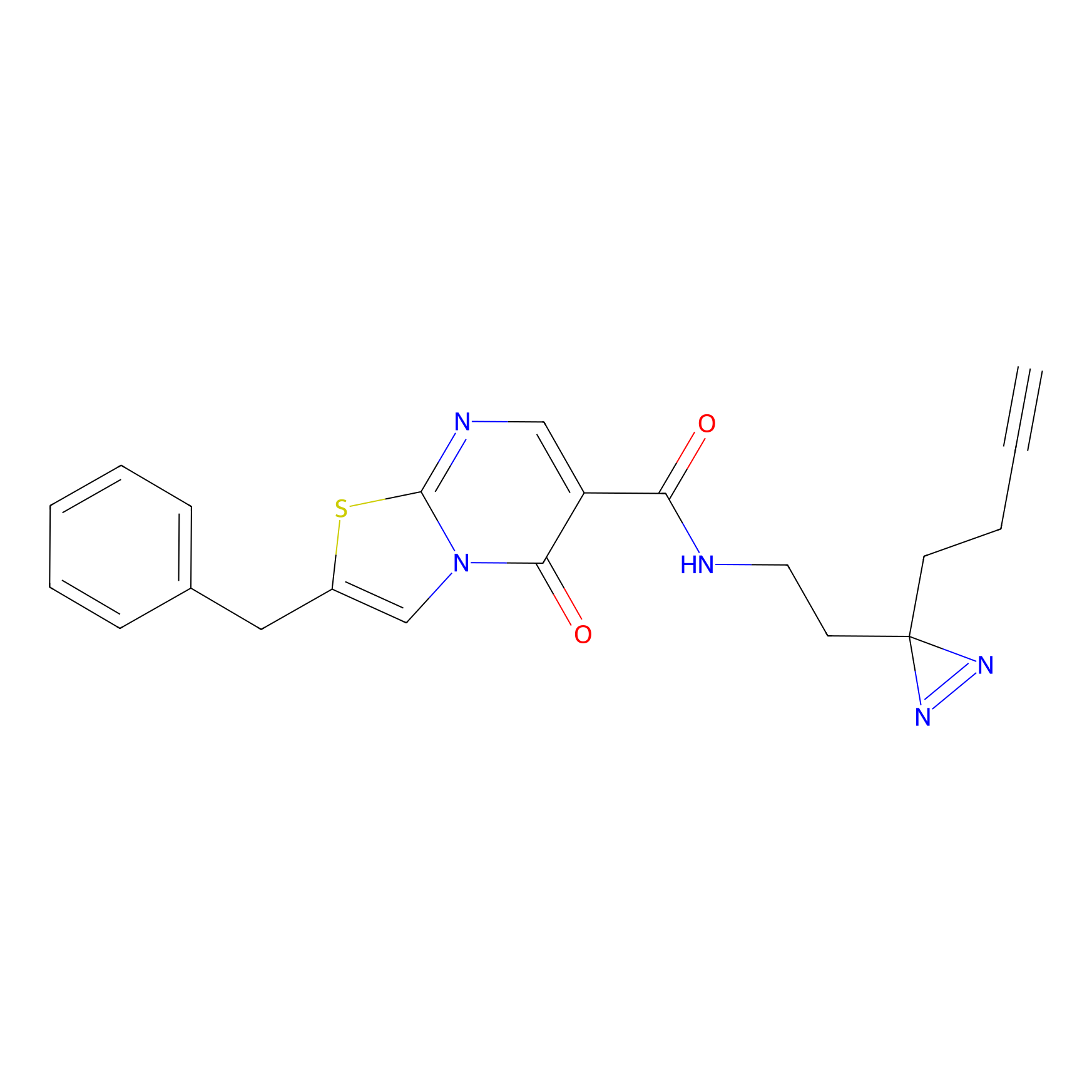
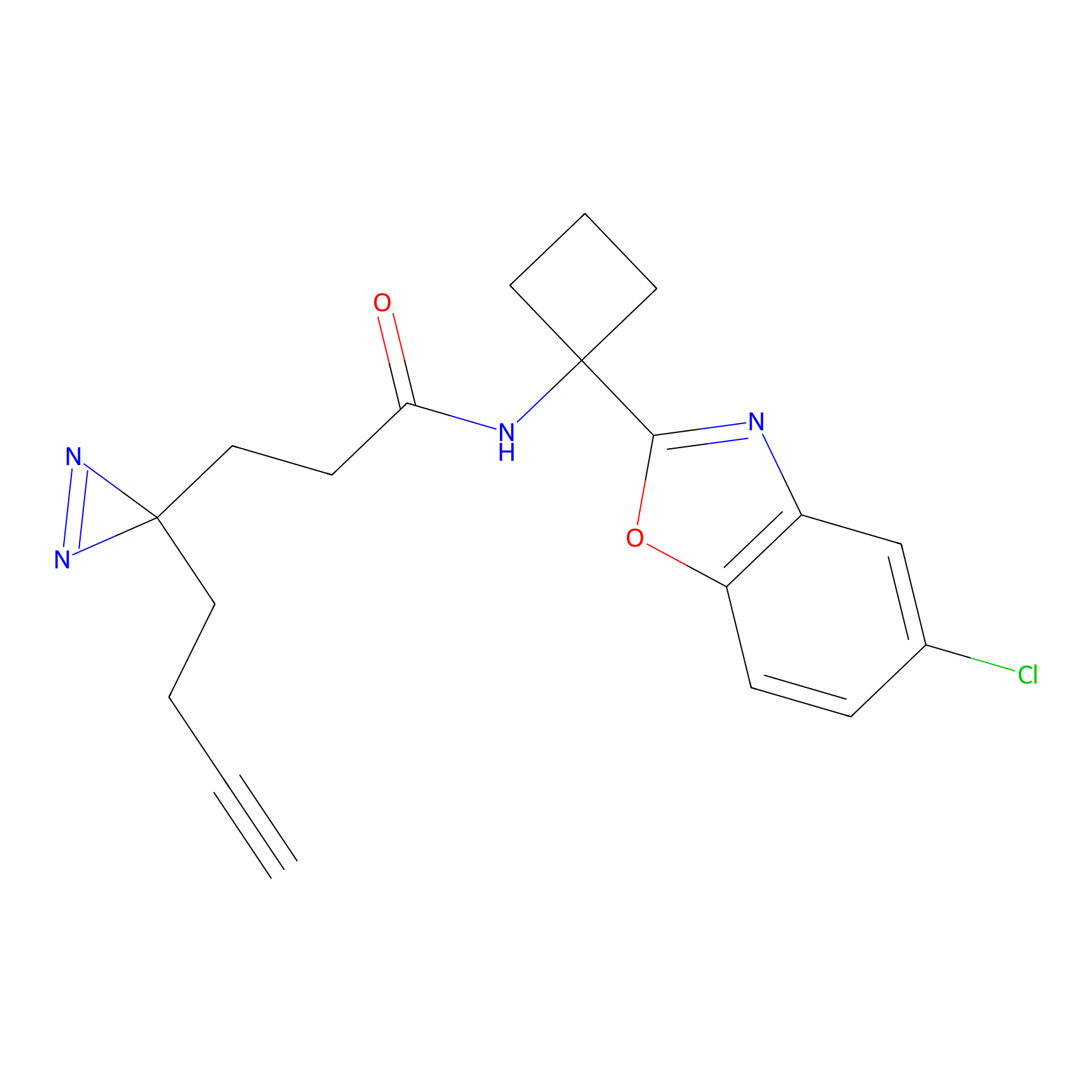
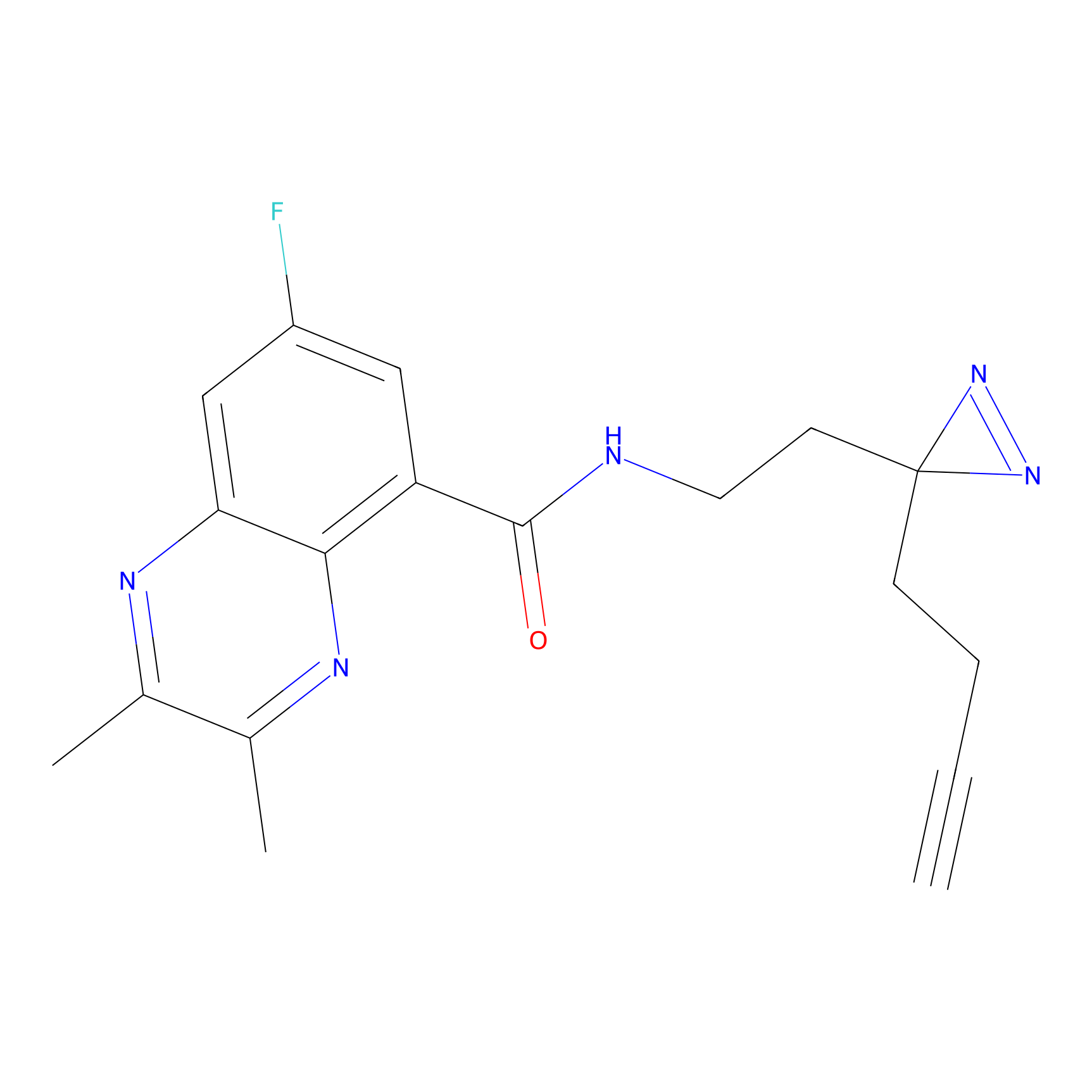
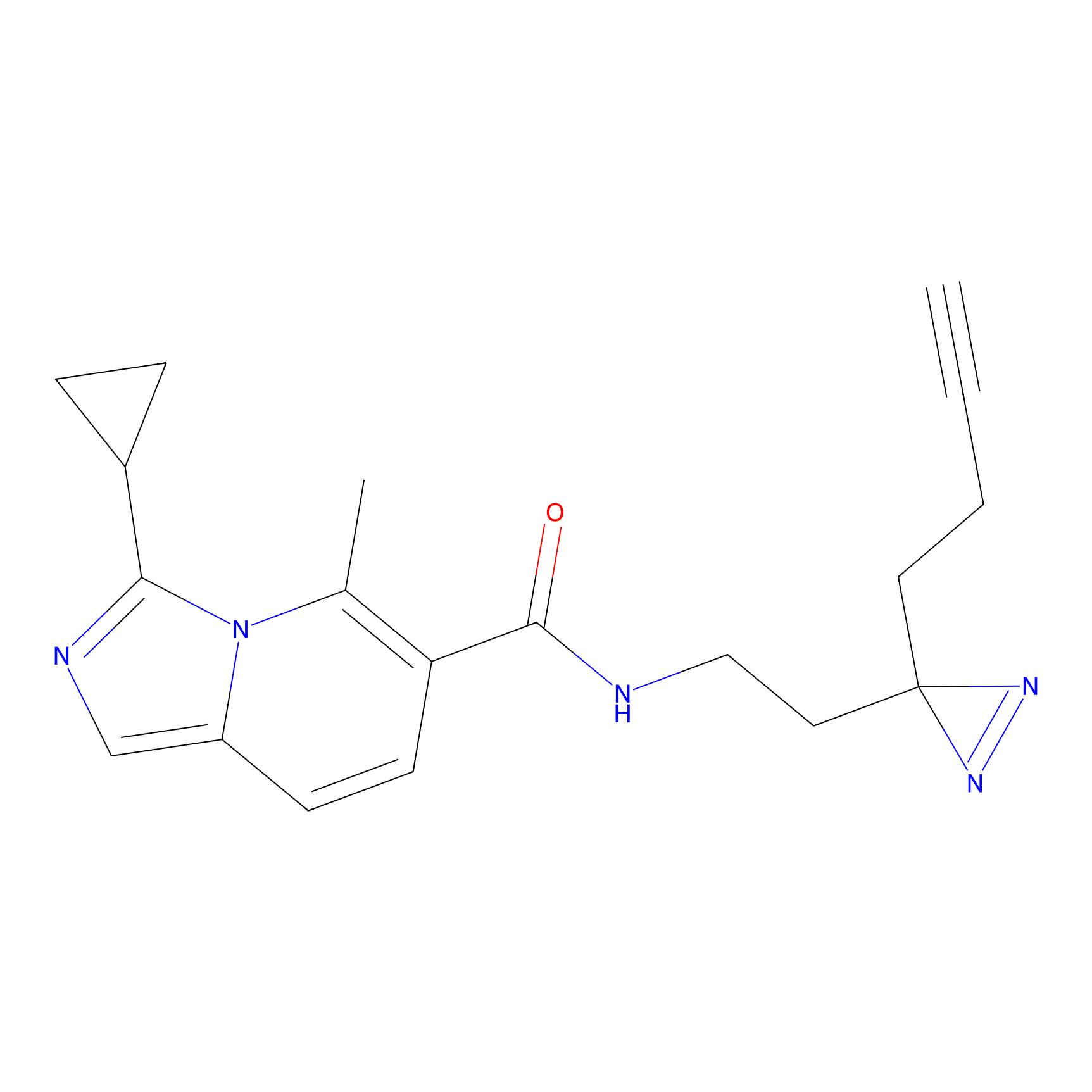
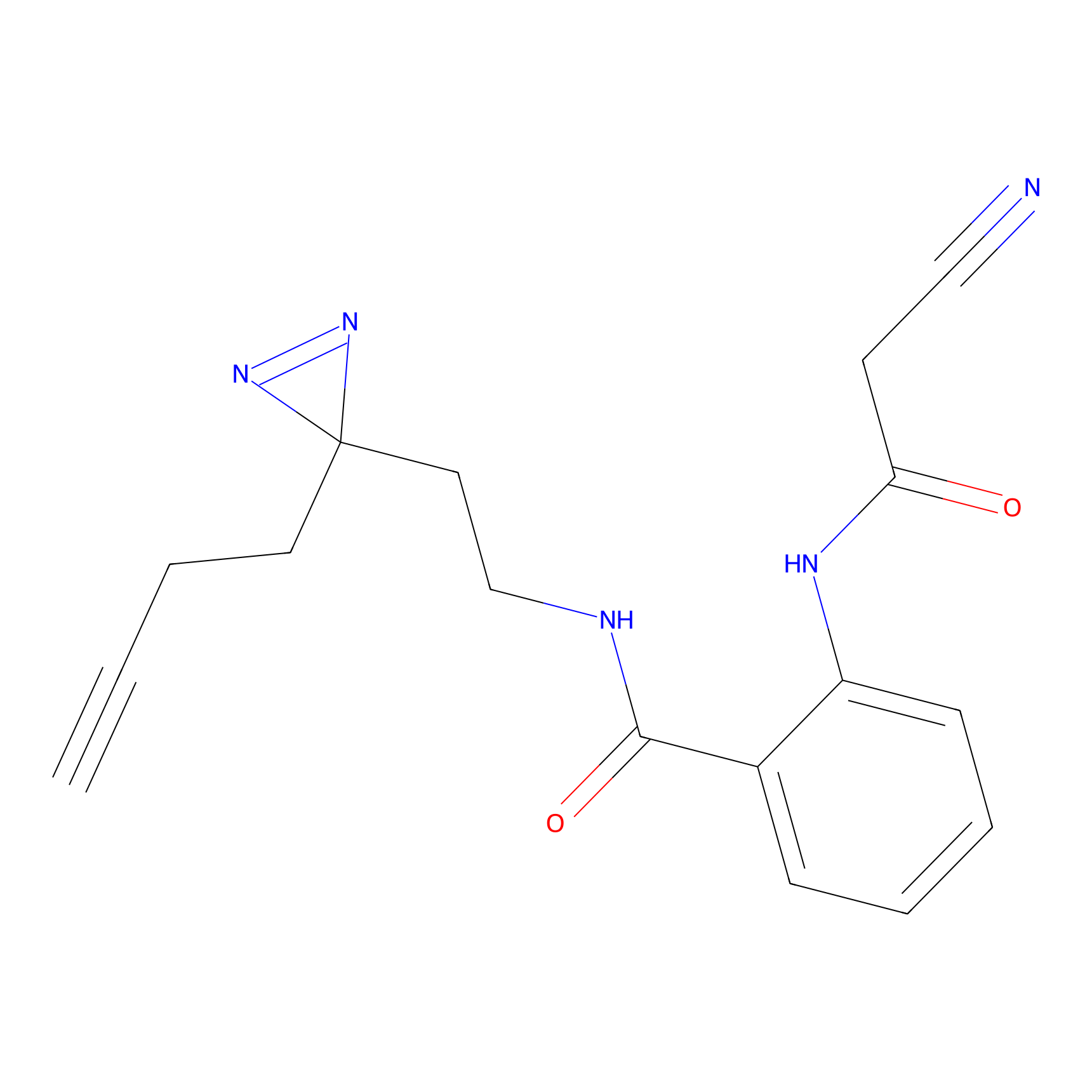
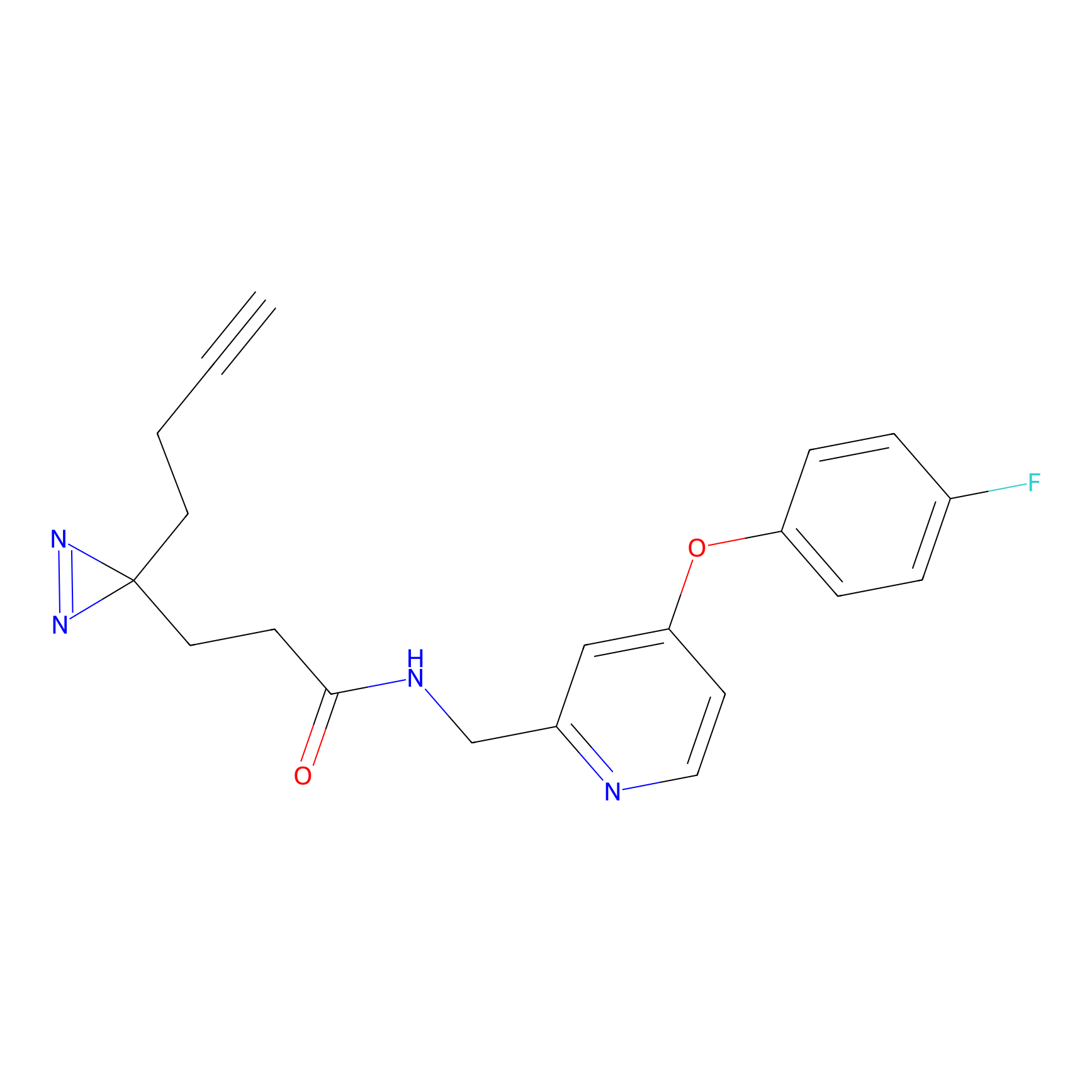
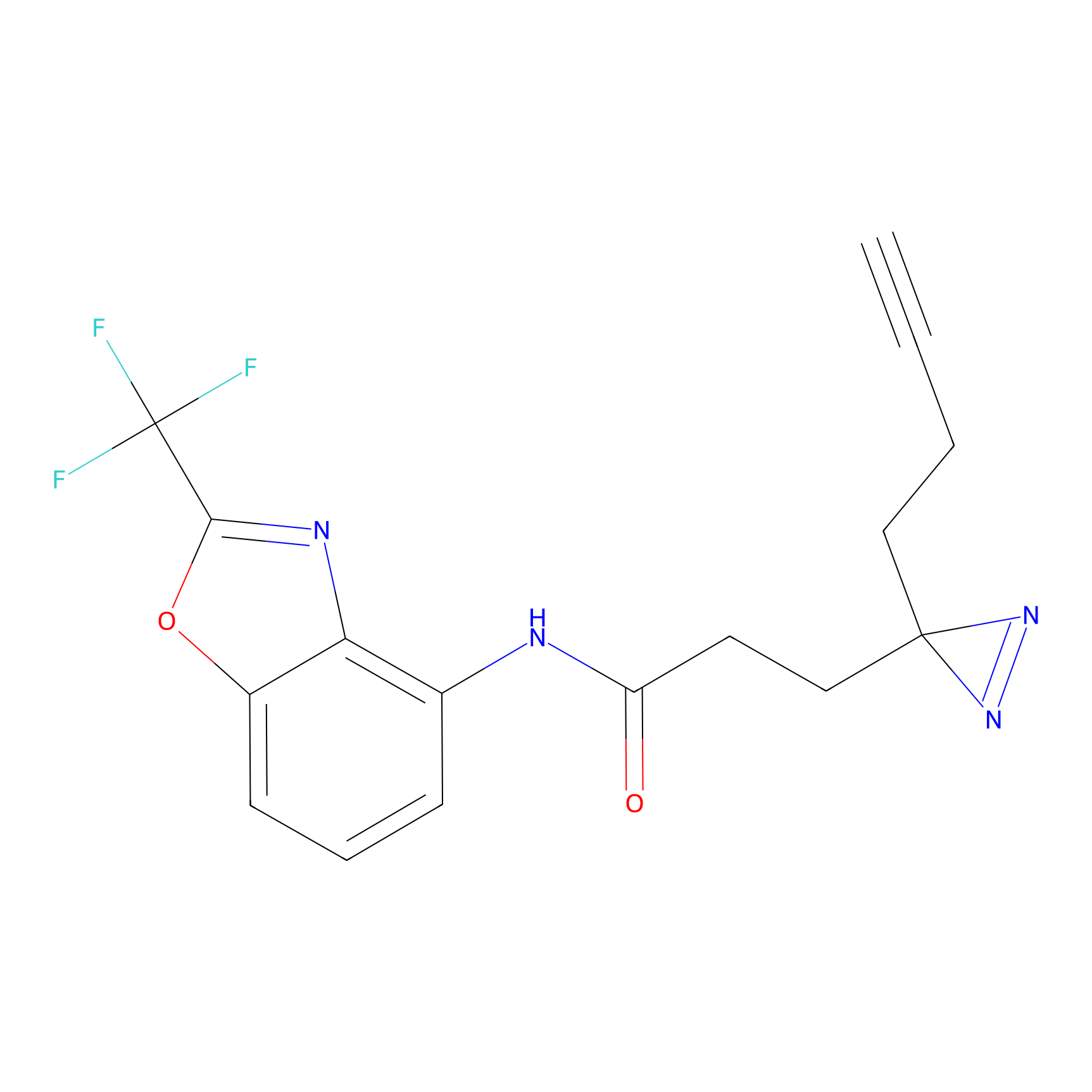
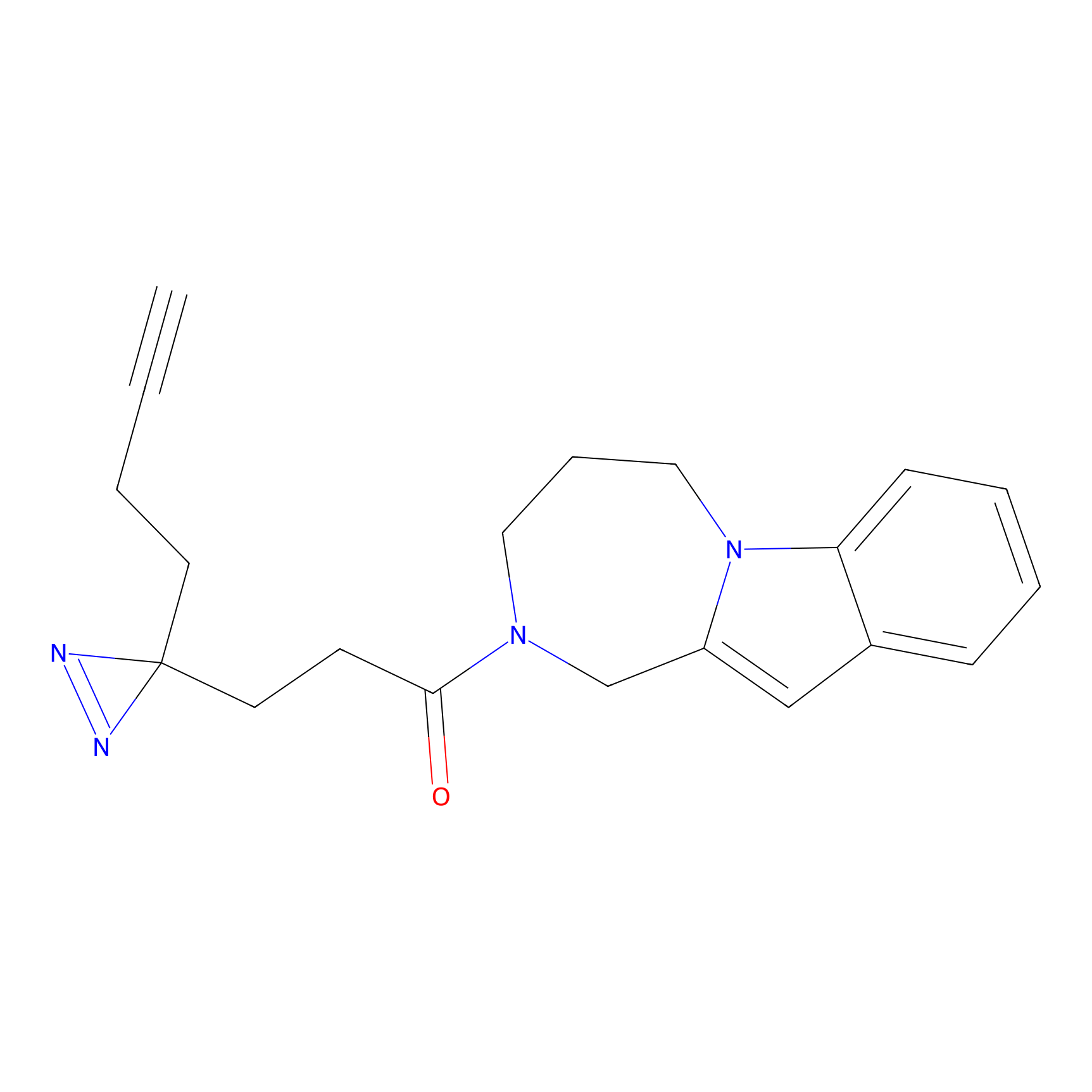
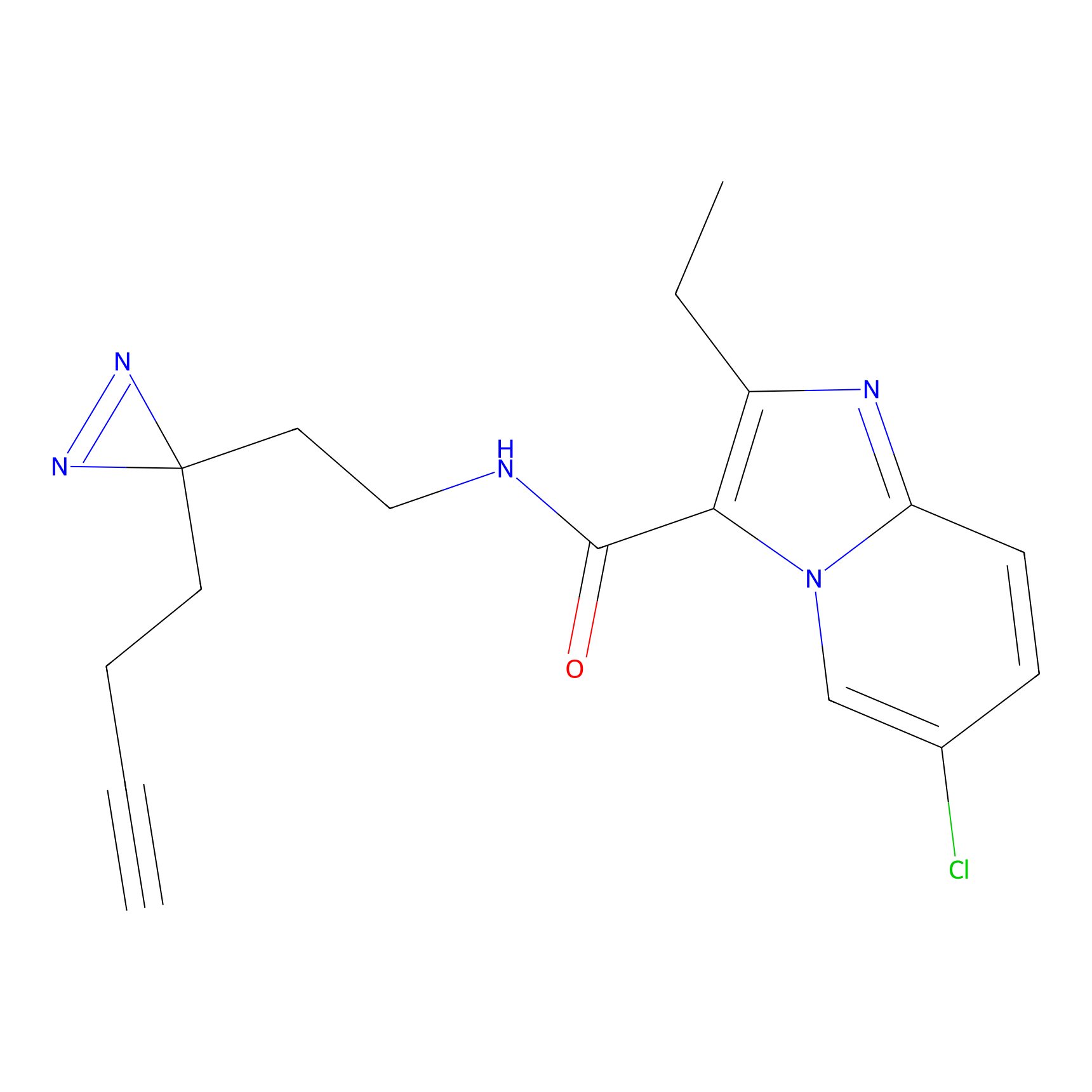
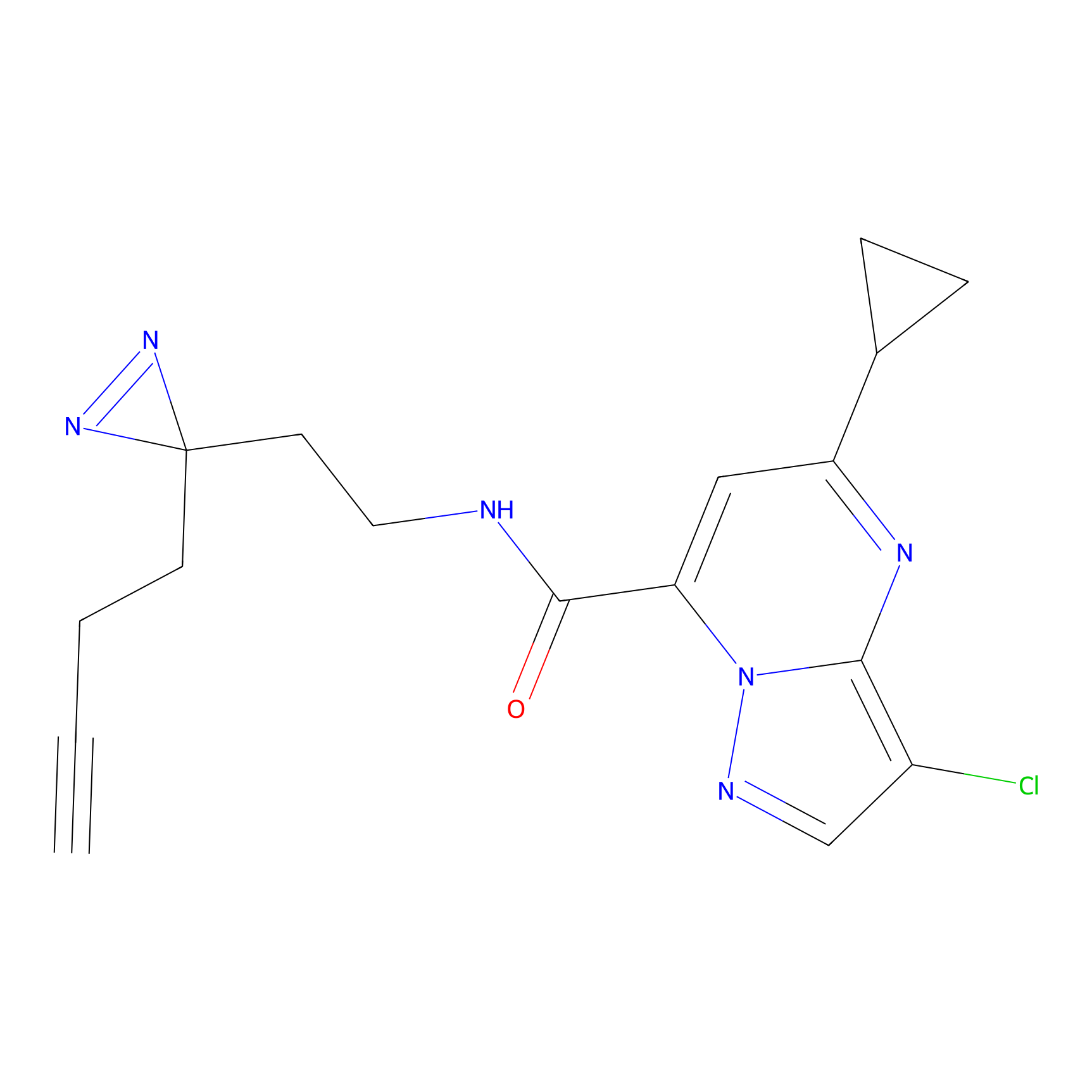
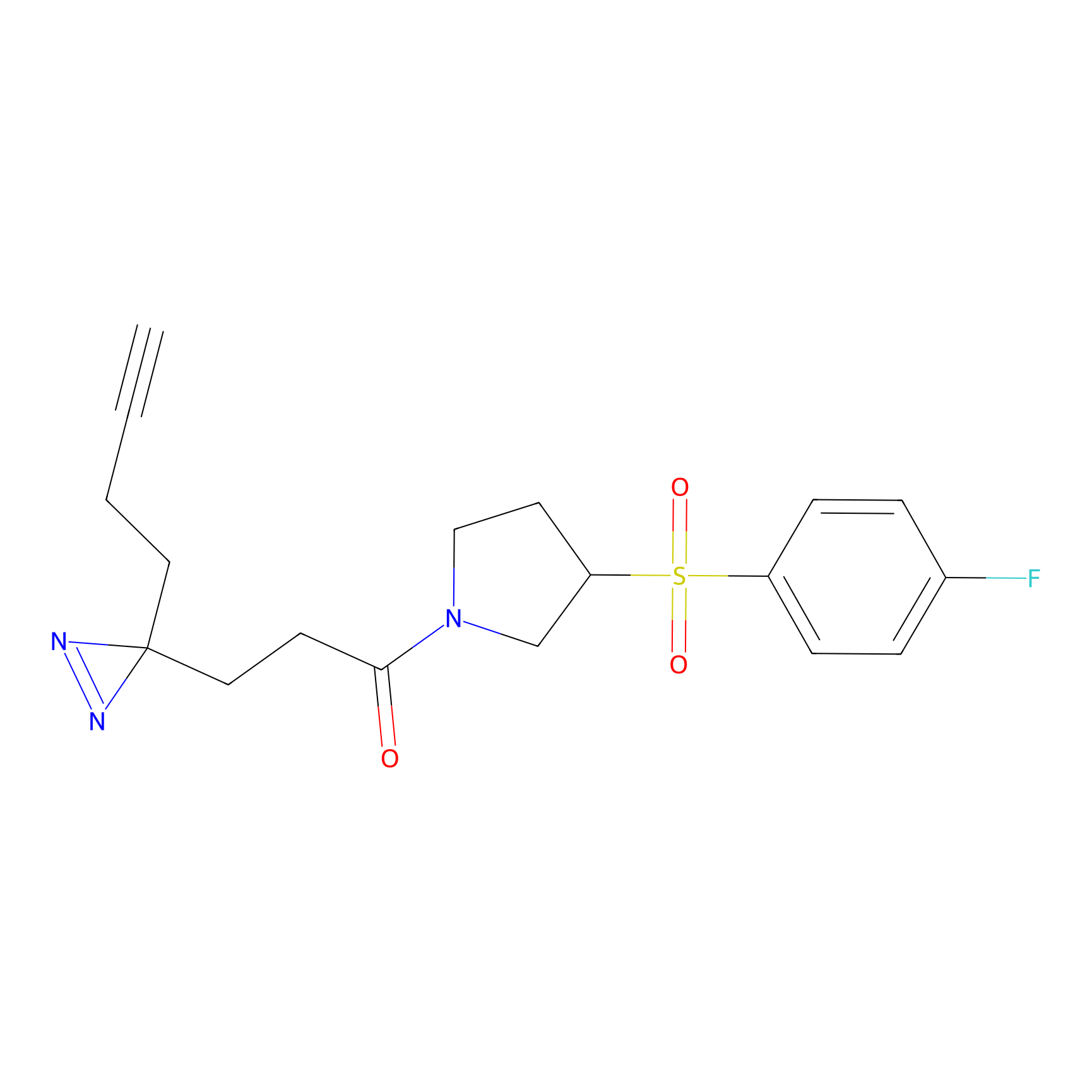
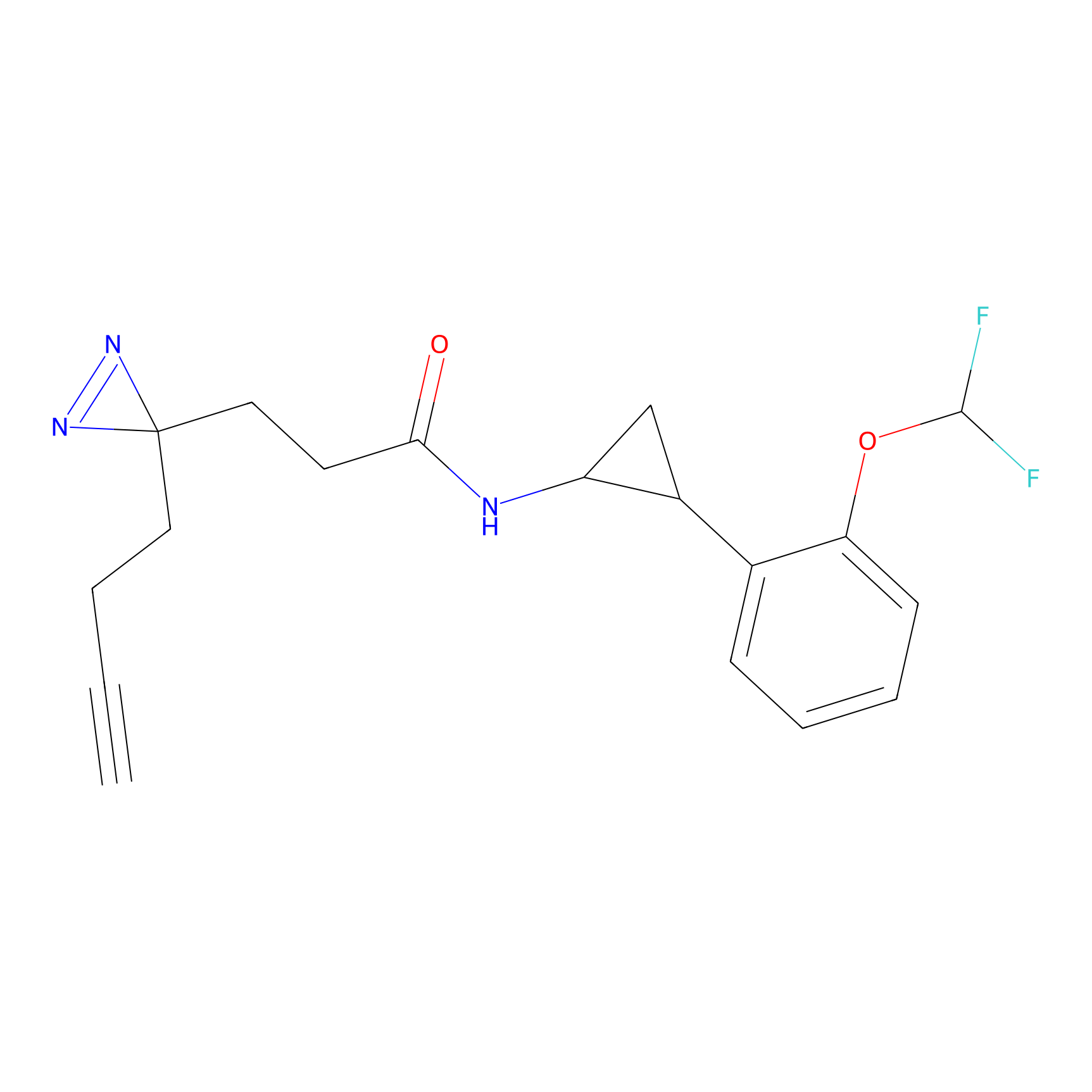
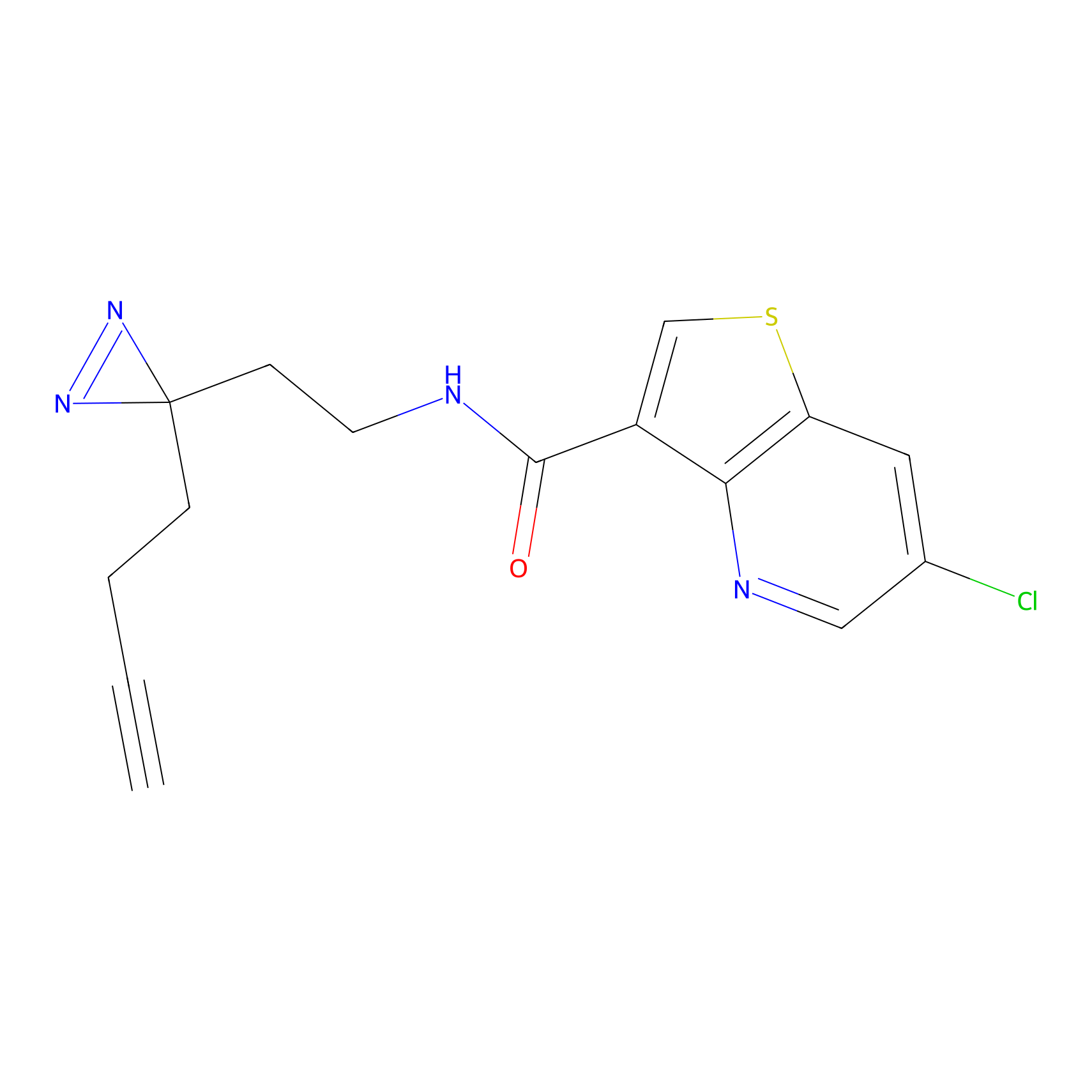
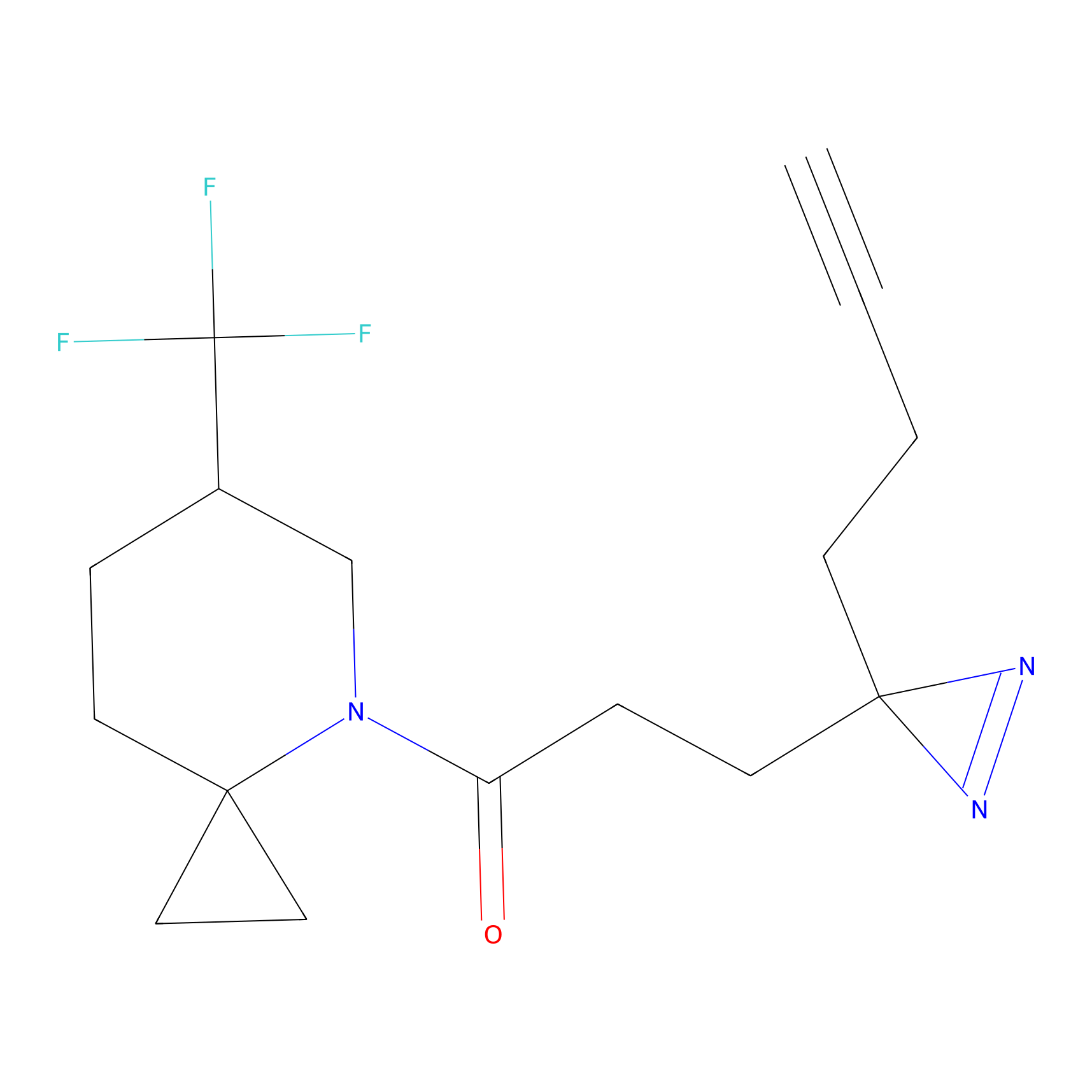
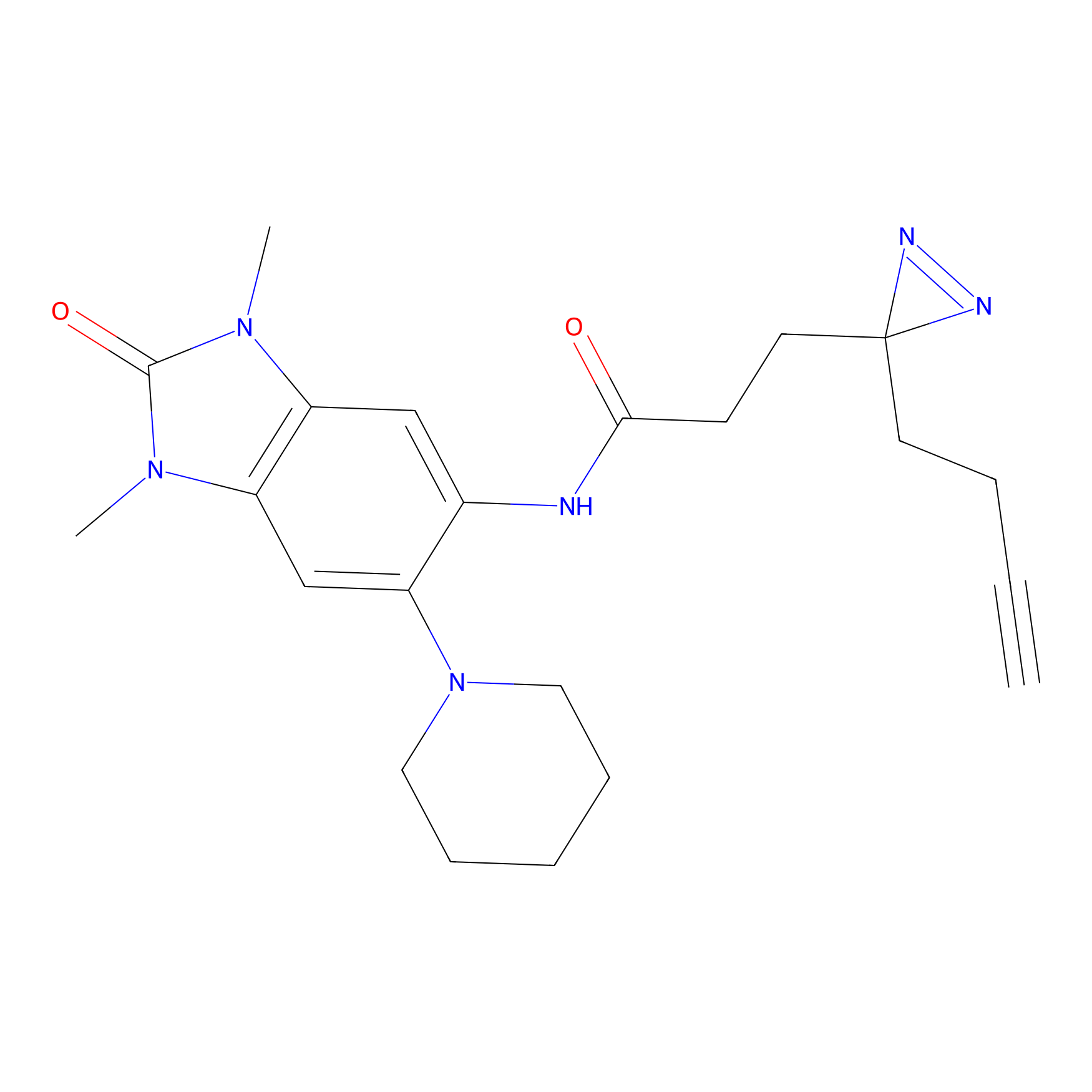
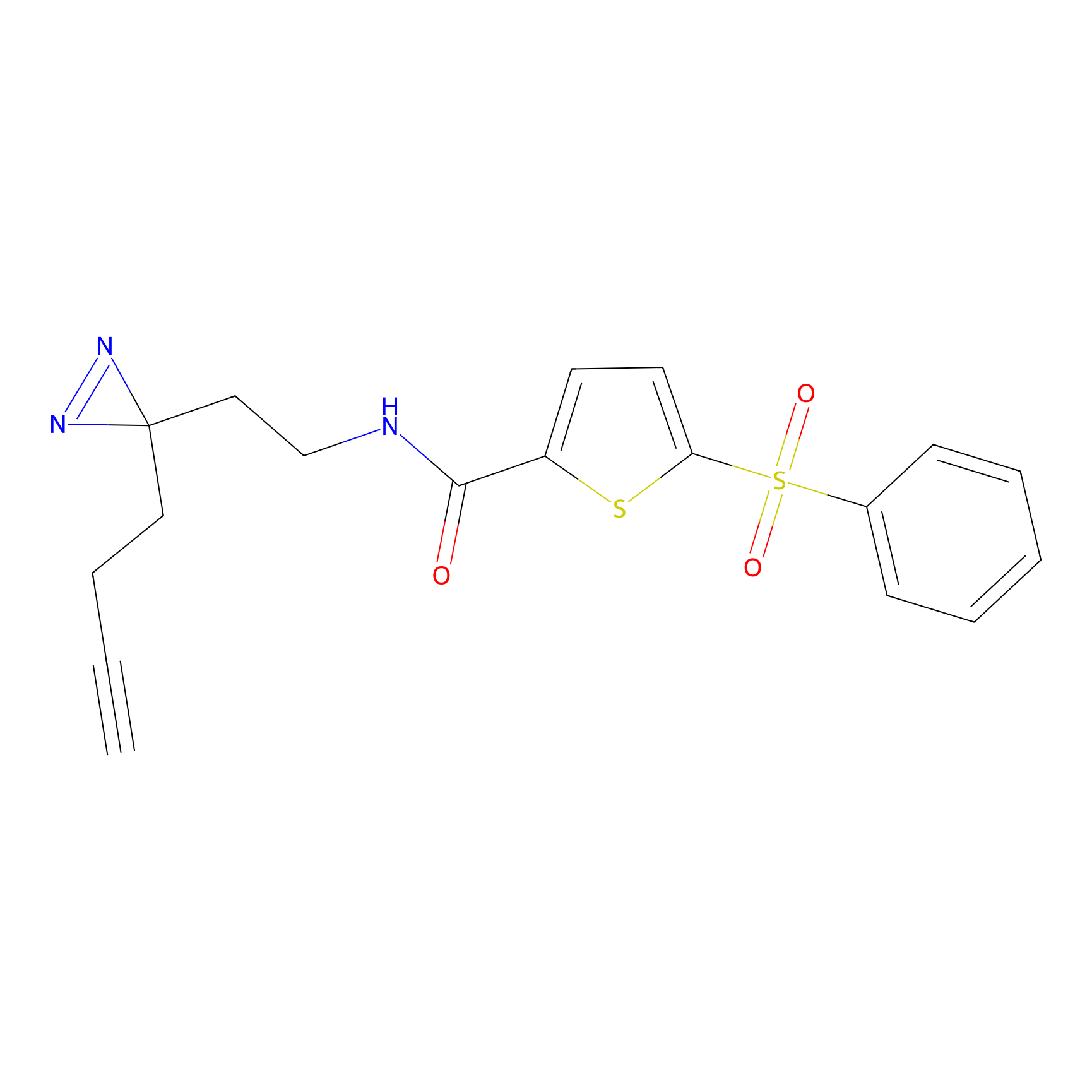
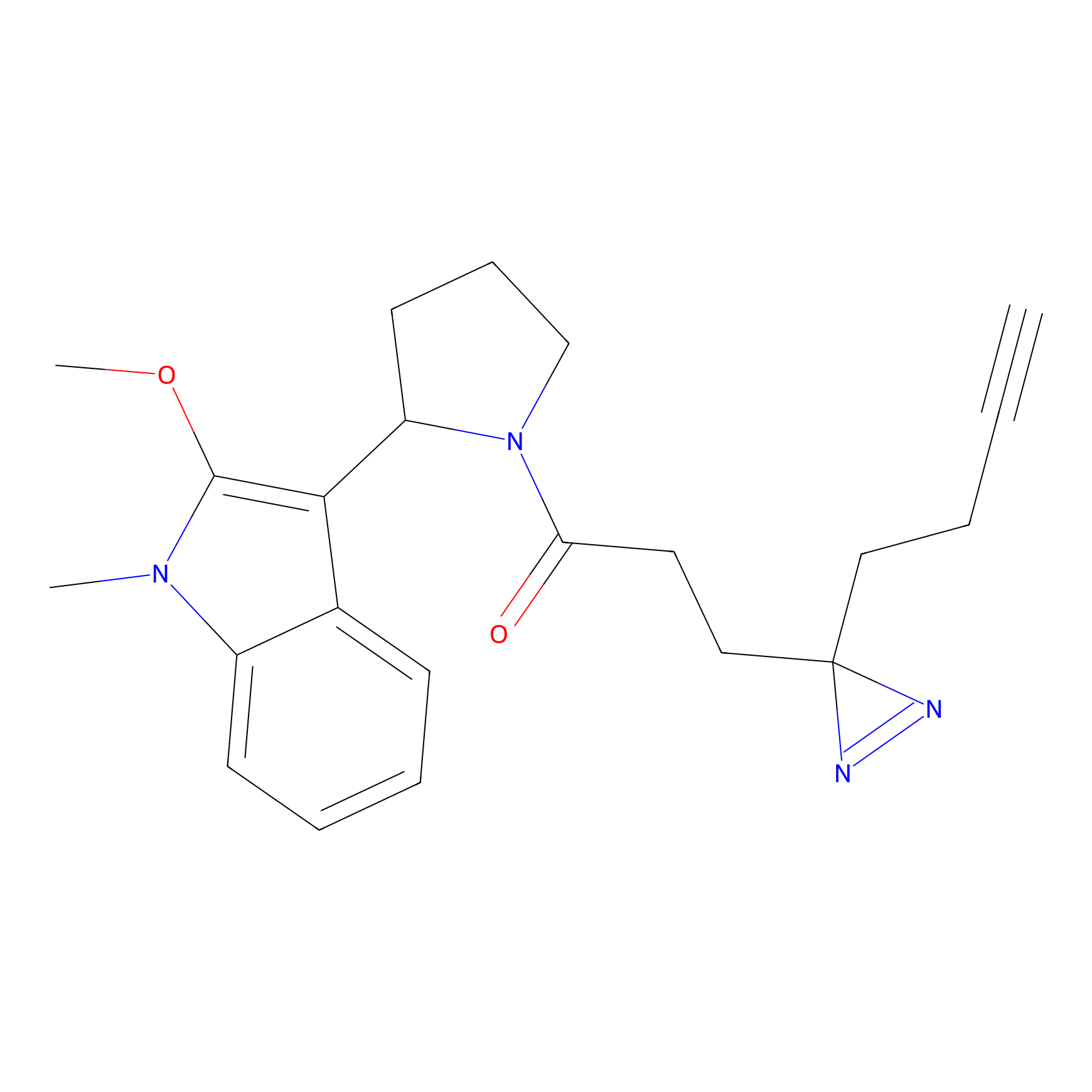
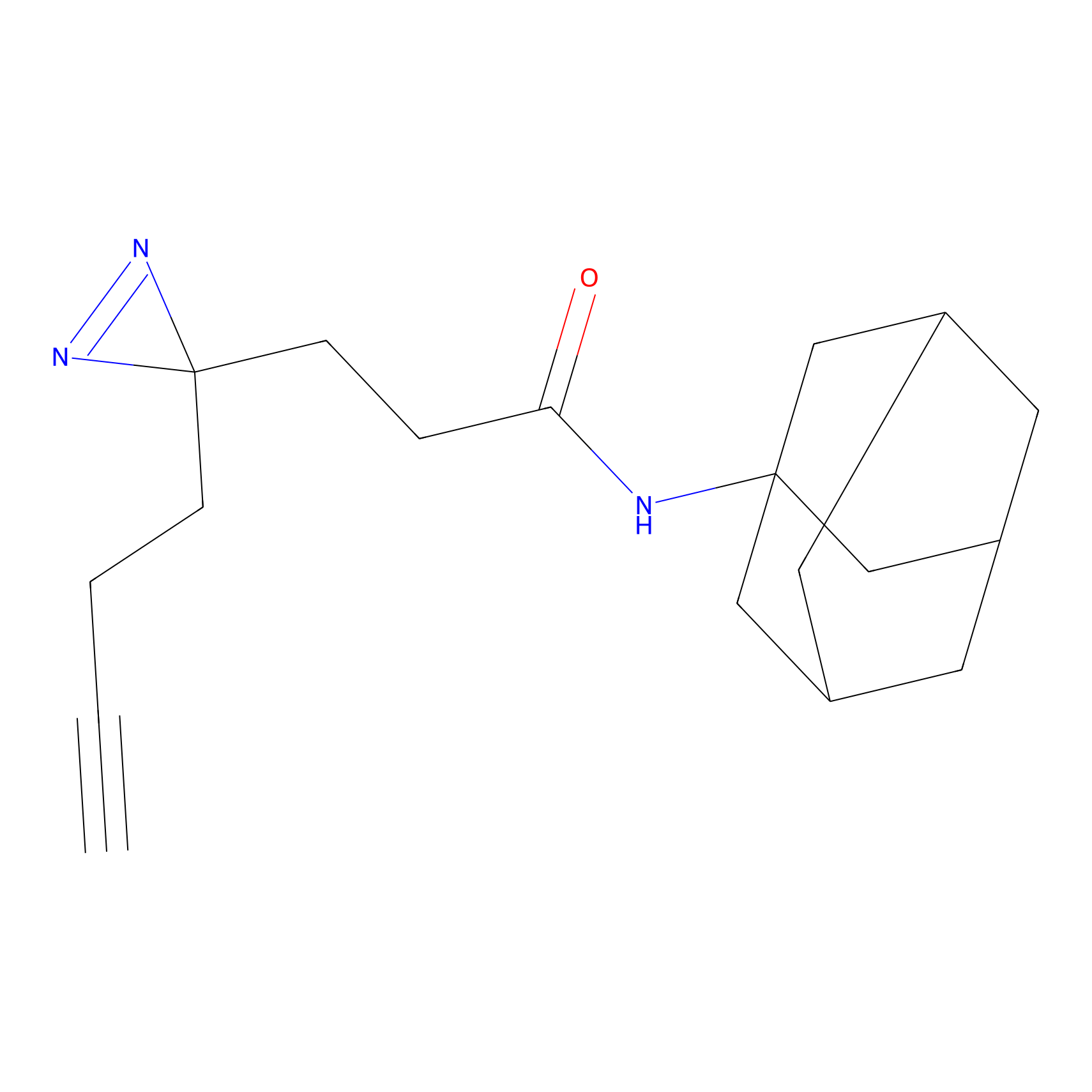
|
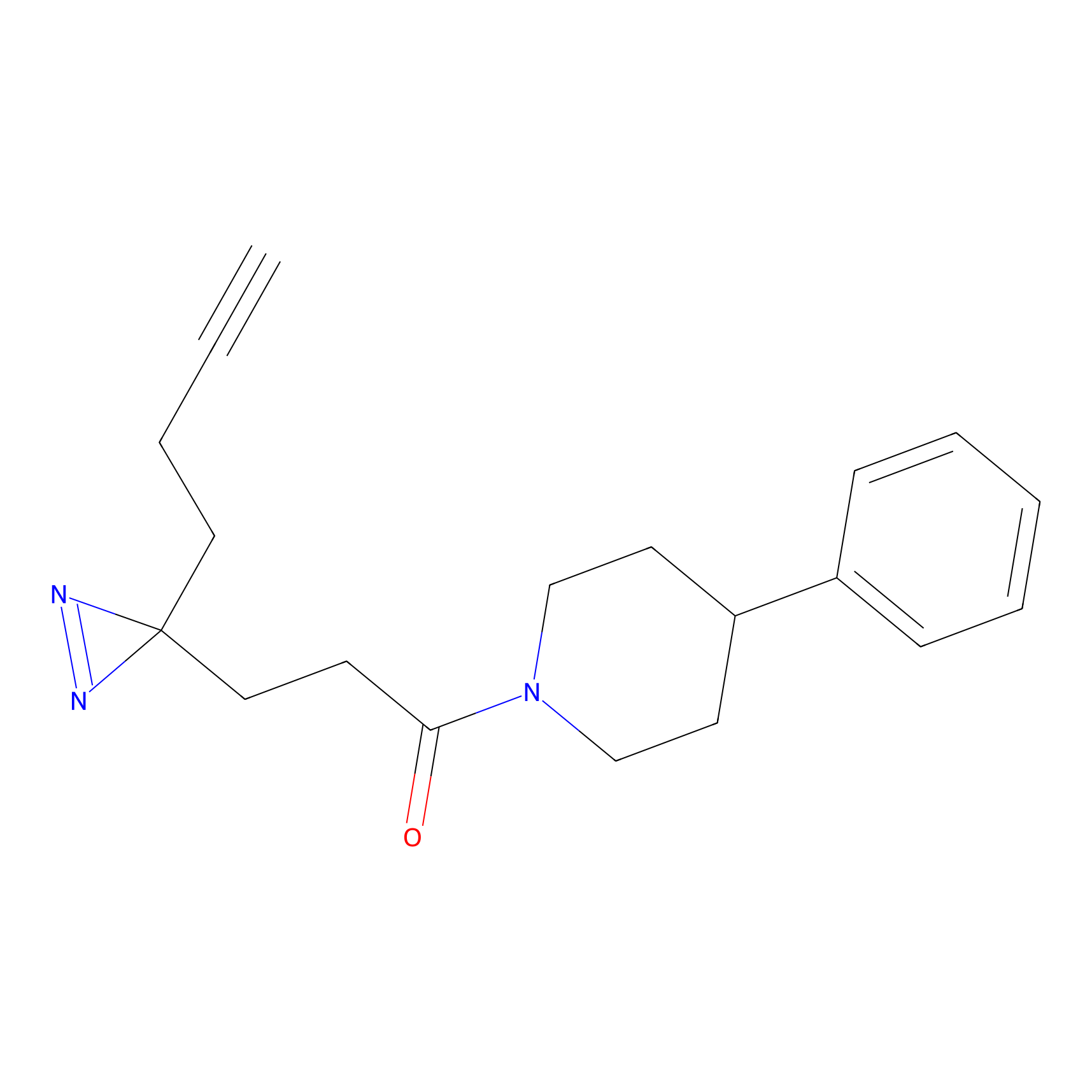
CHEMBL5175495 Probe Info |
 |
5.36 | LDD0196 | [1] | |
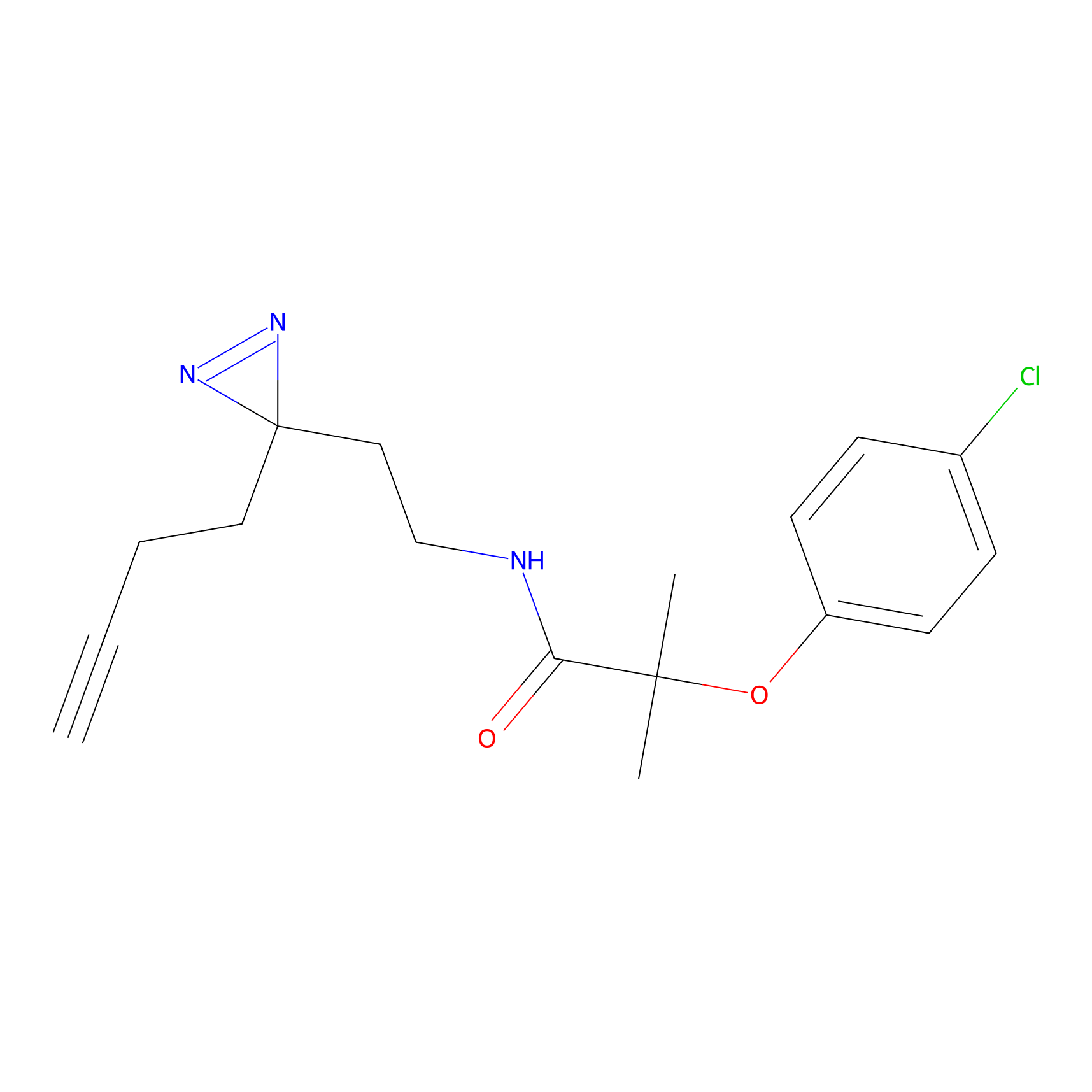
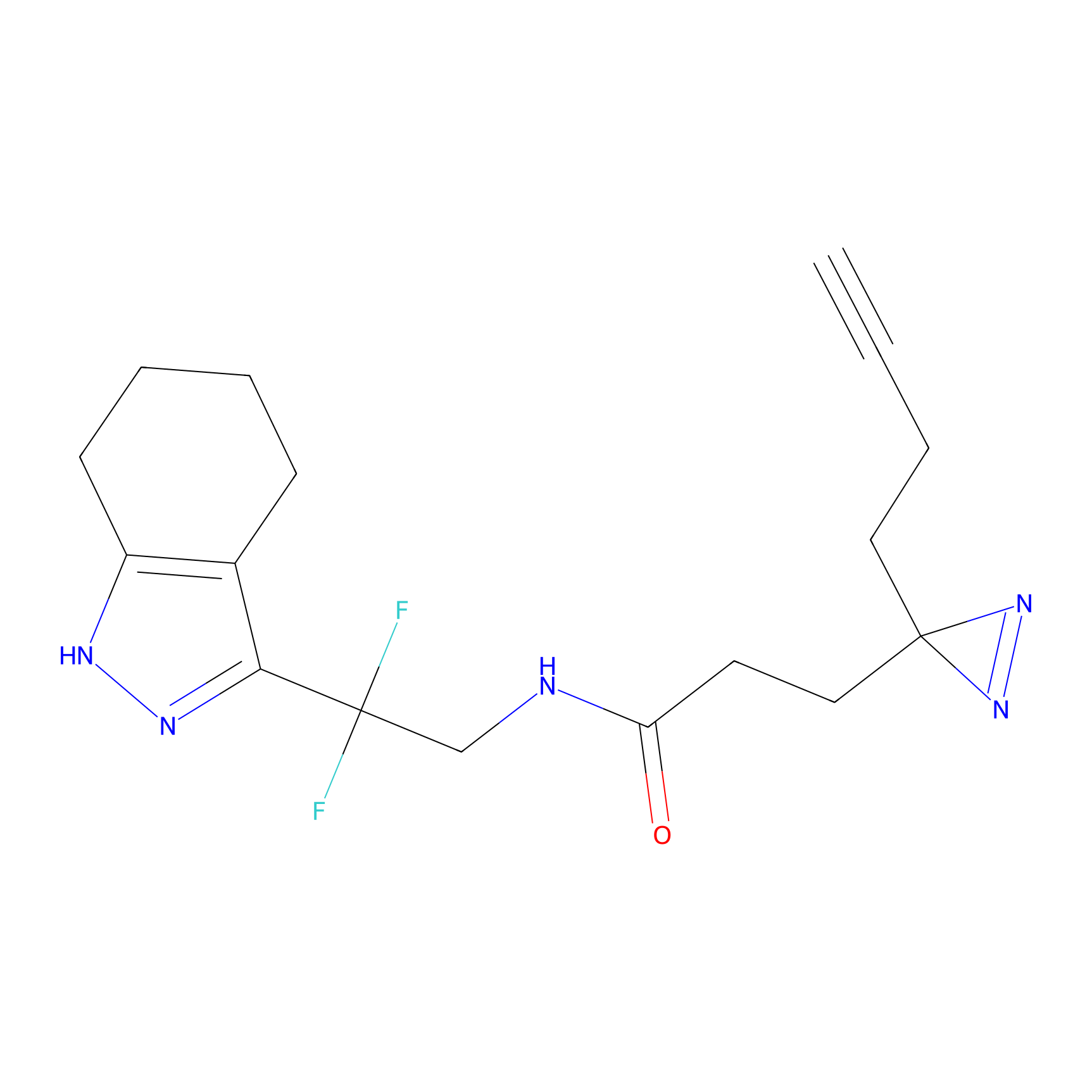
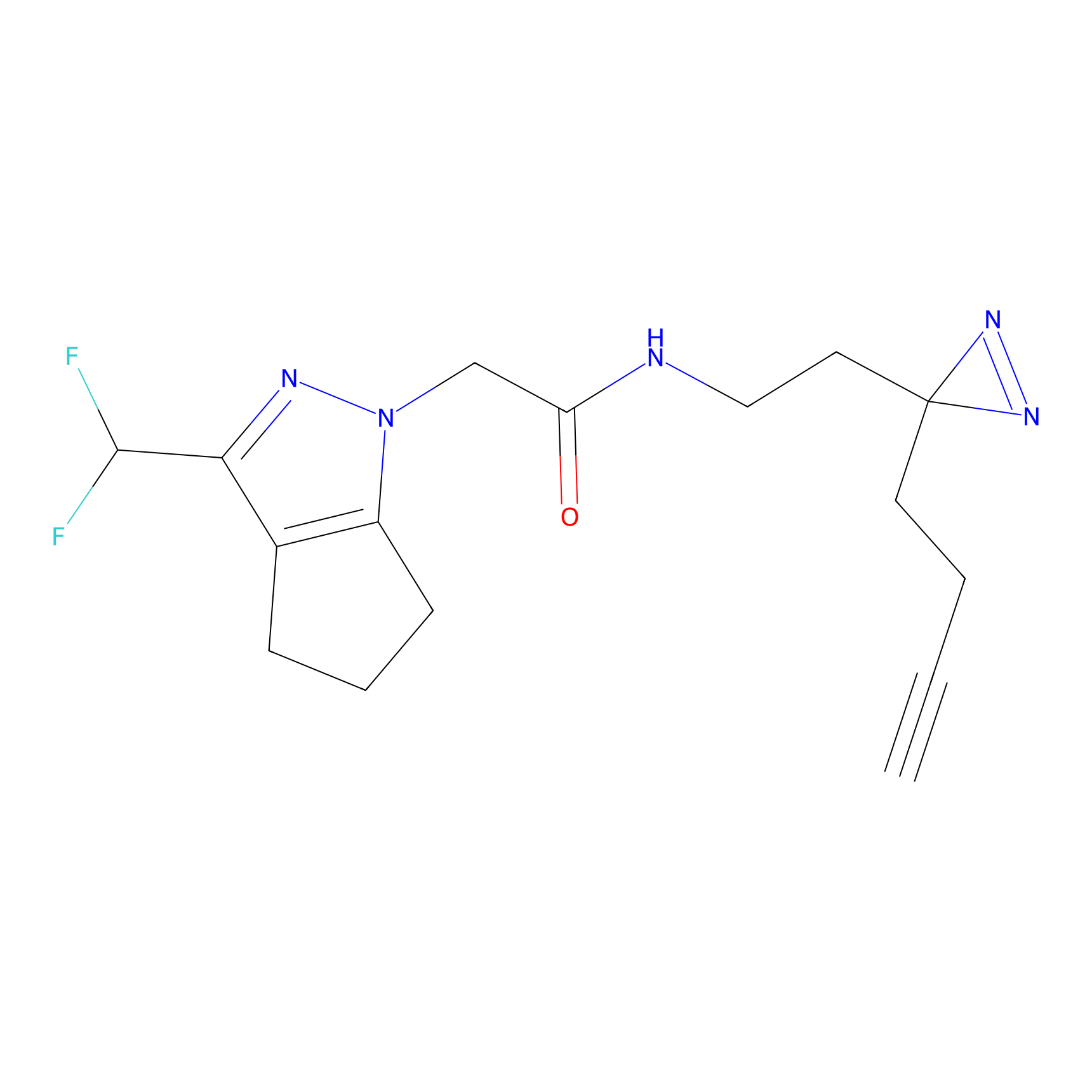
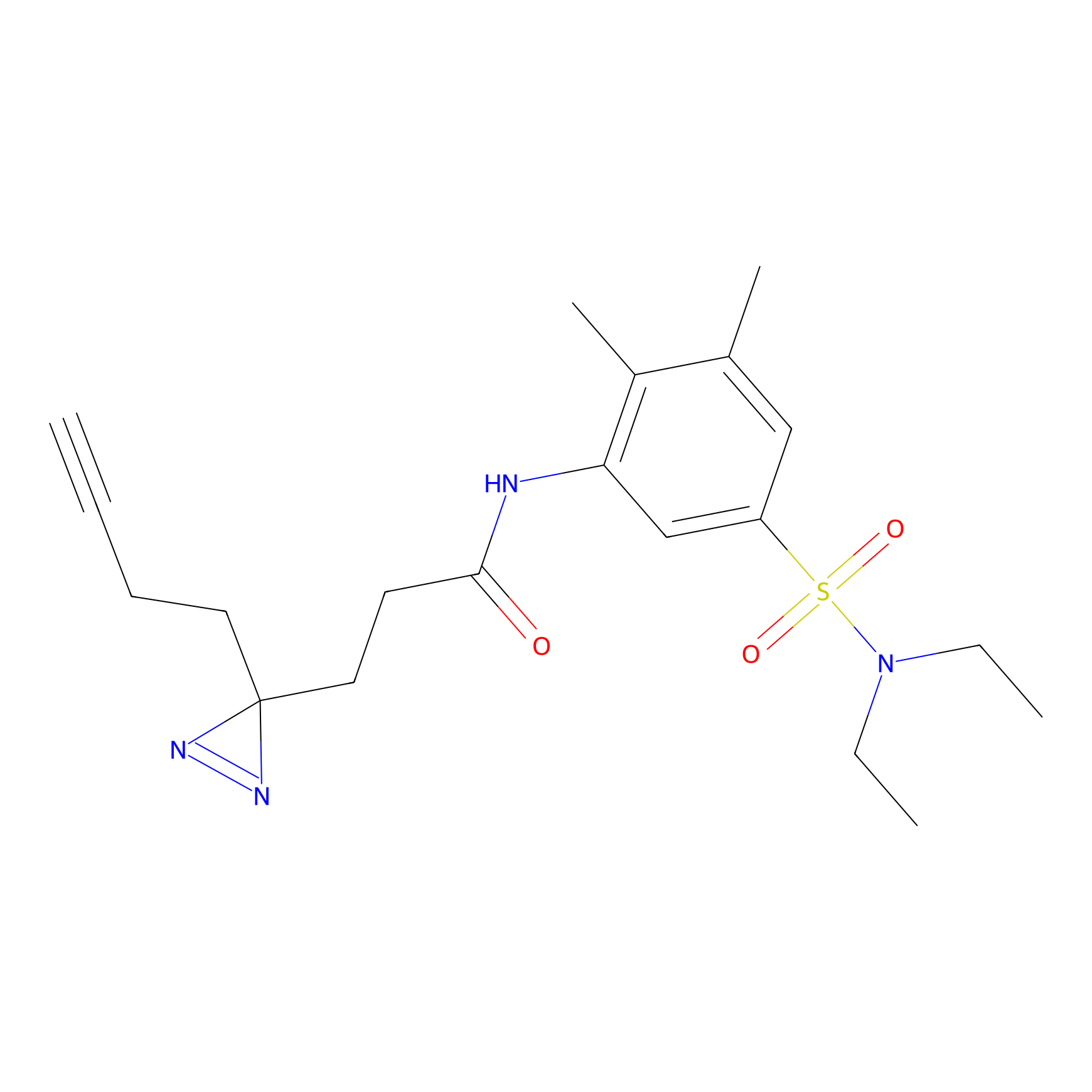
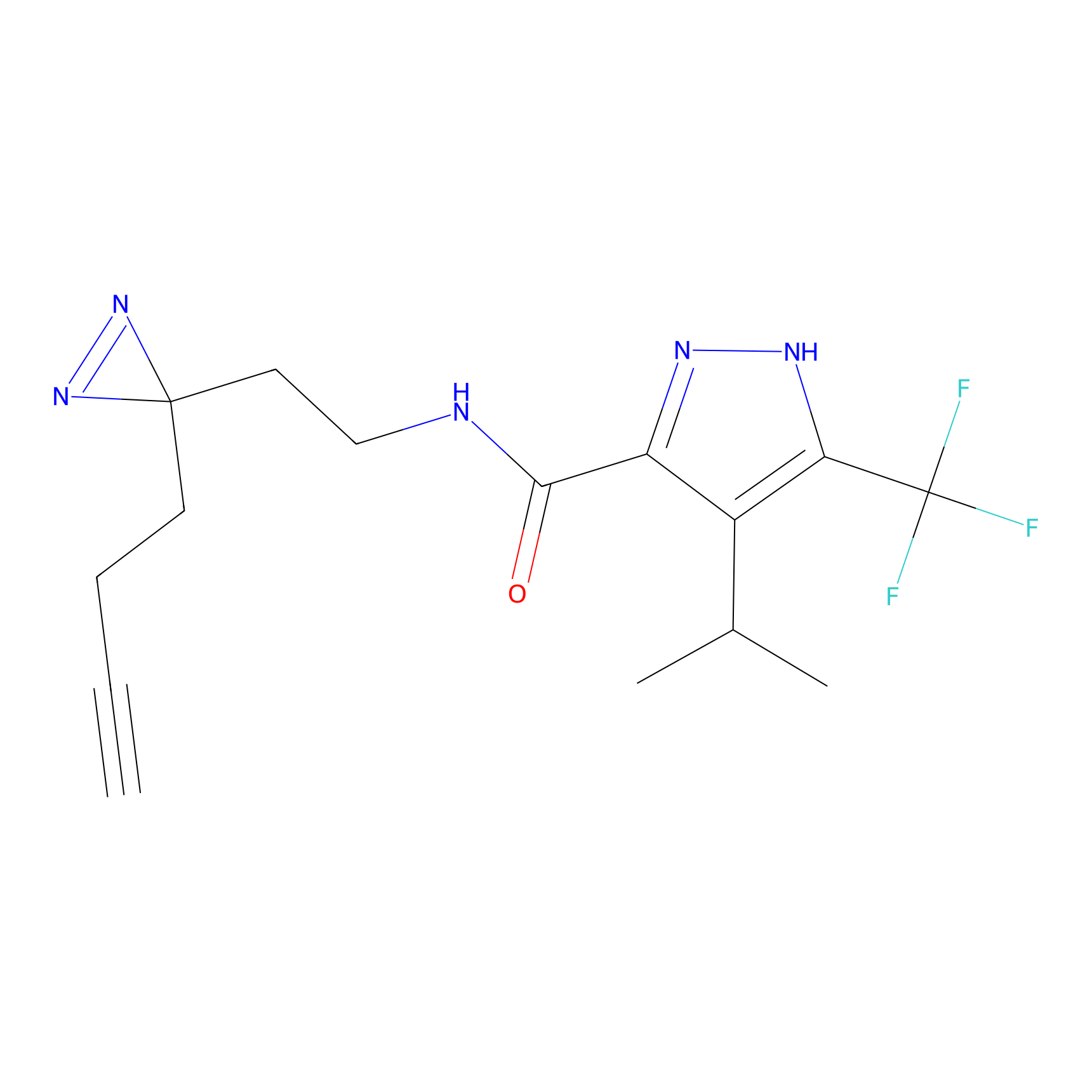
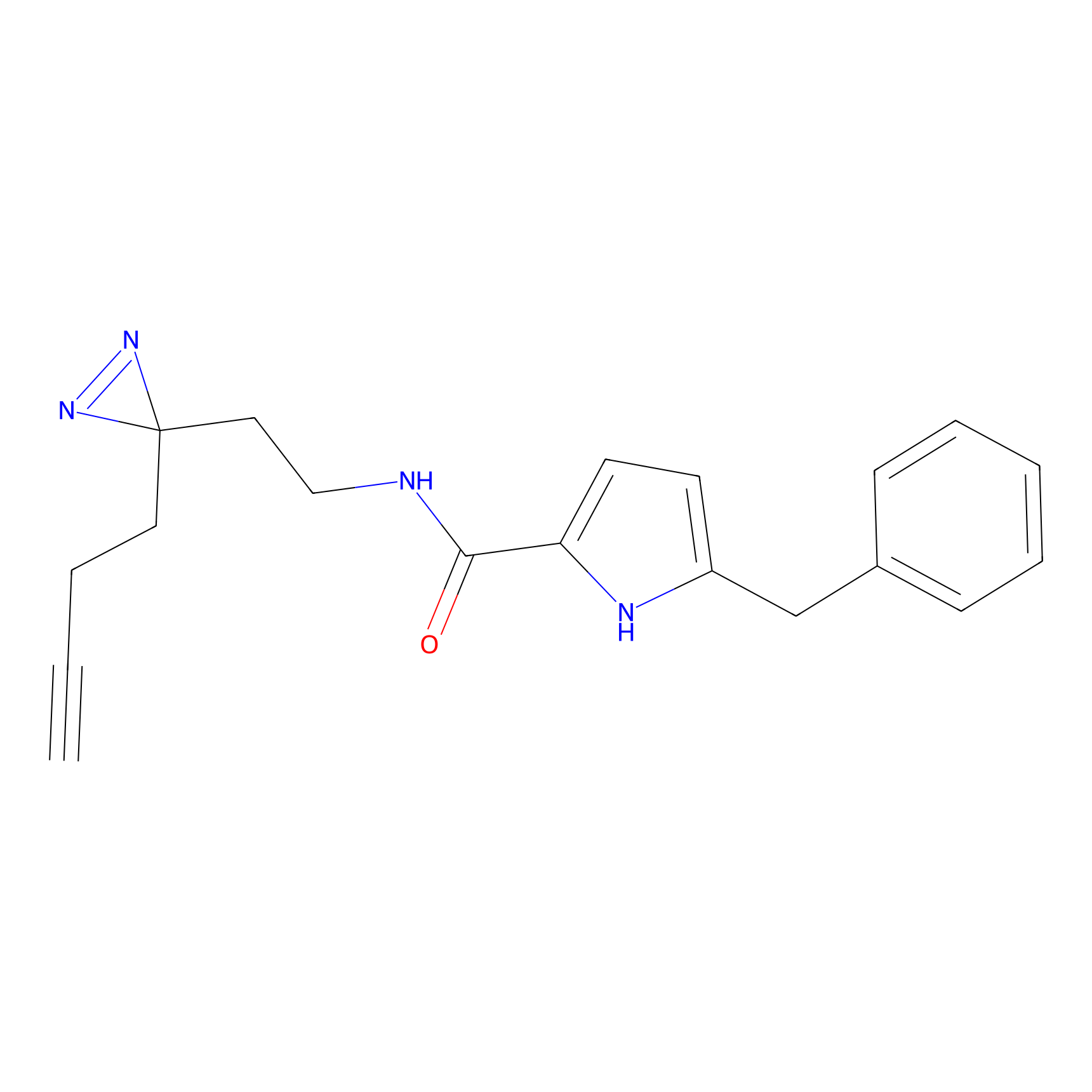
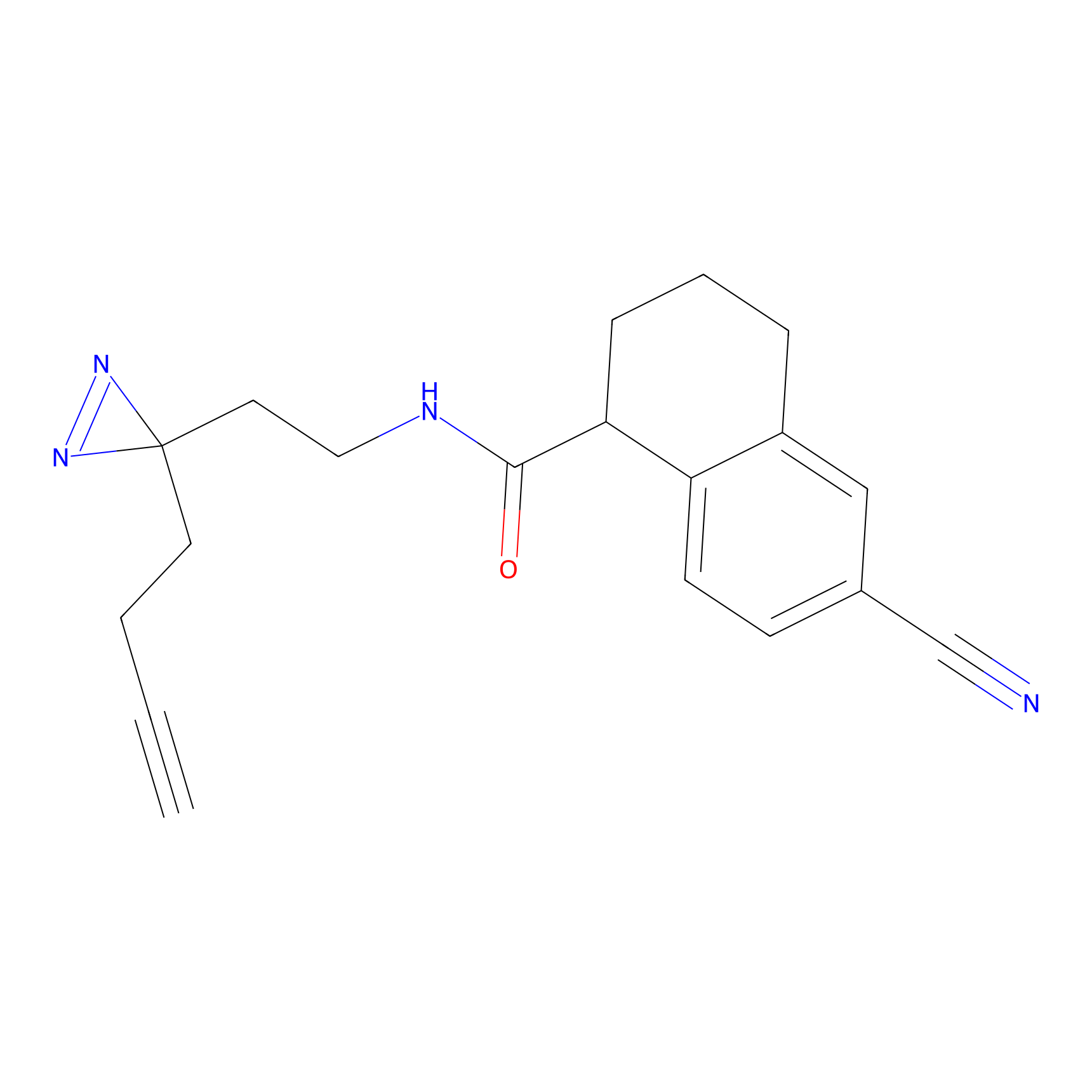
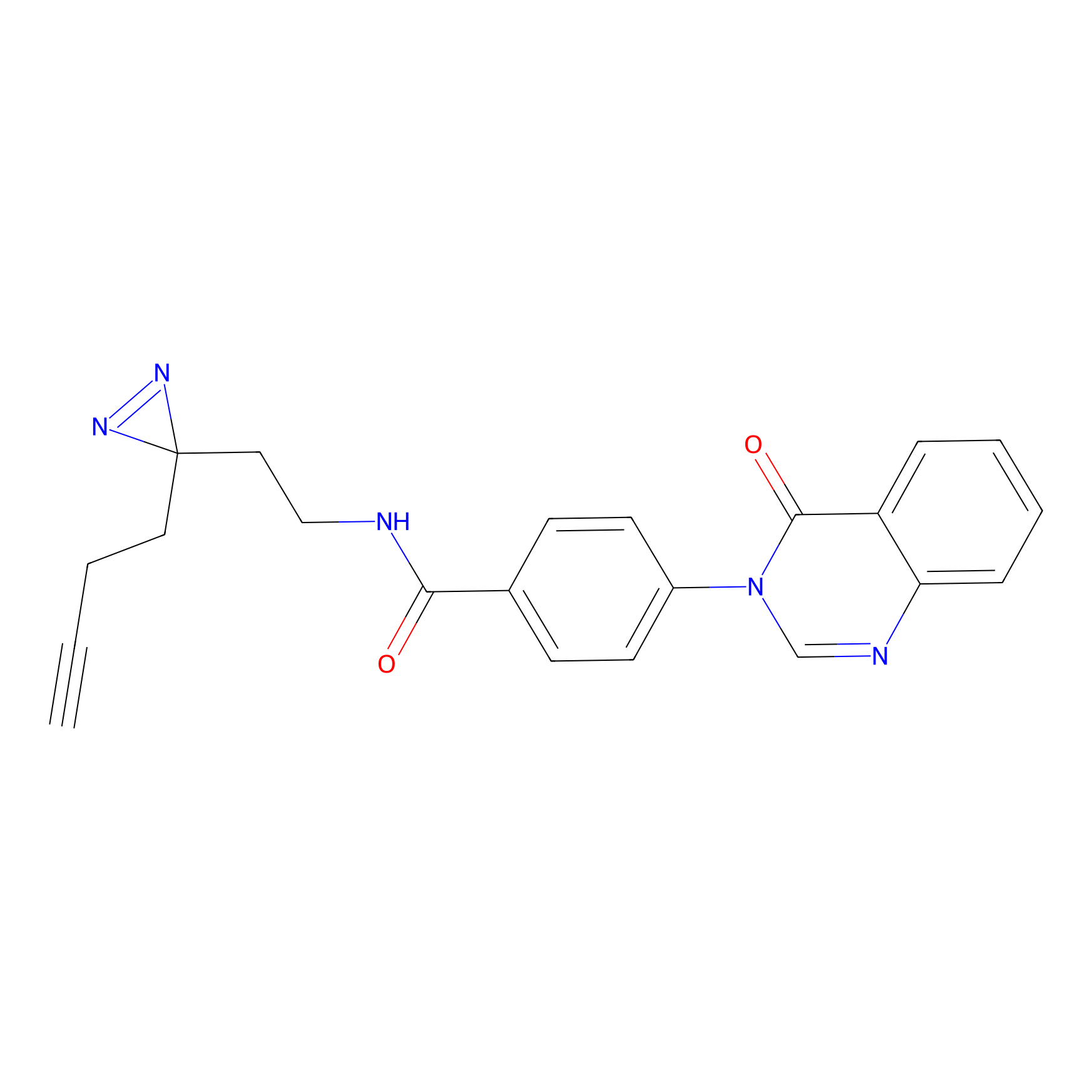
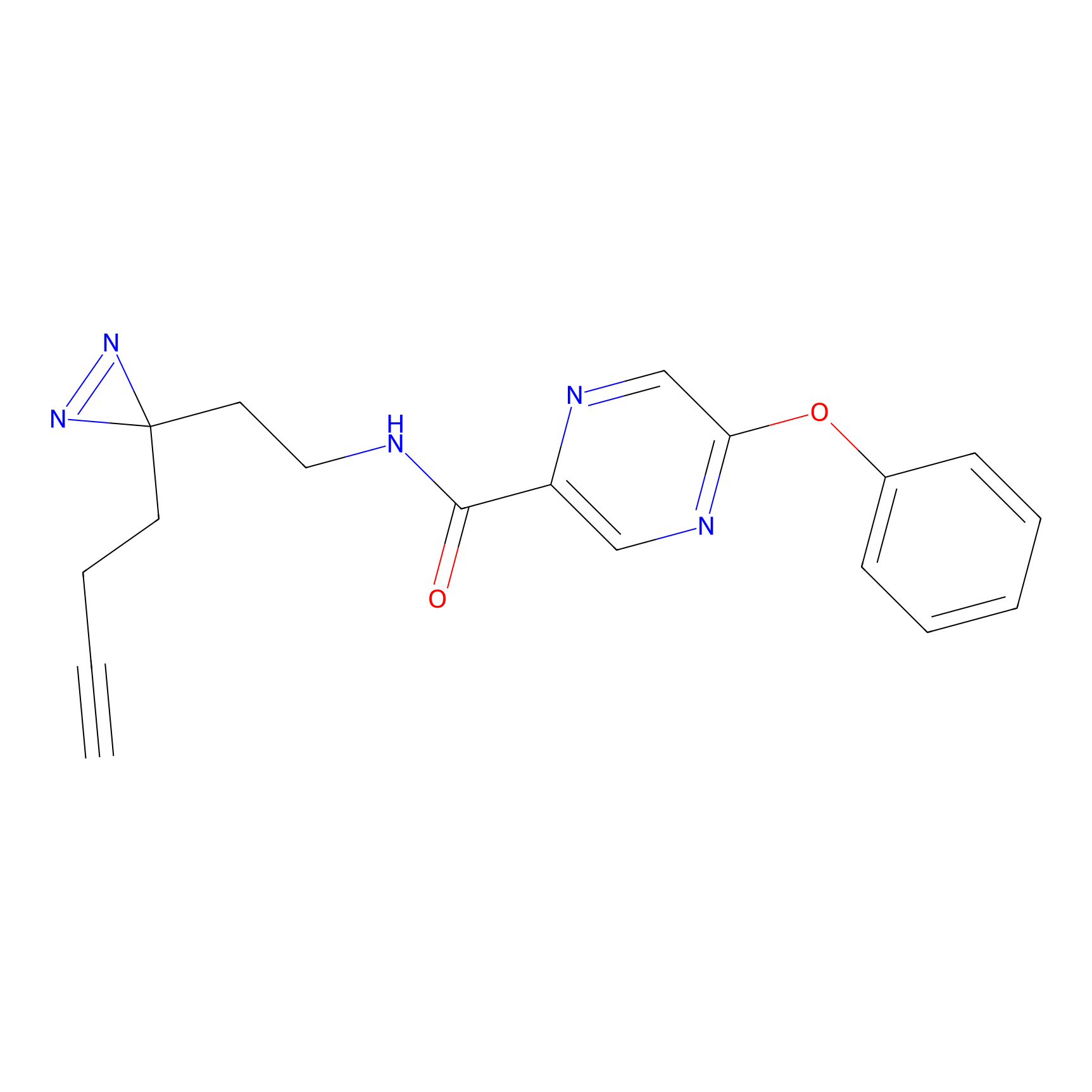
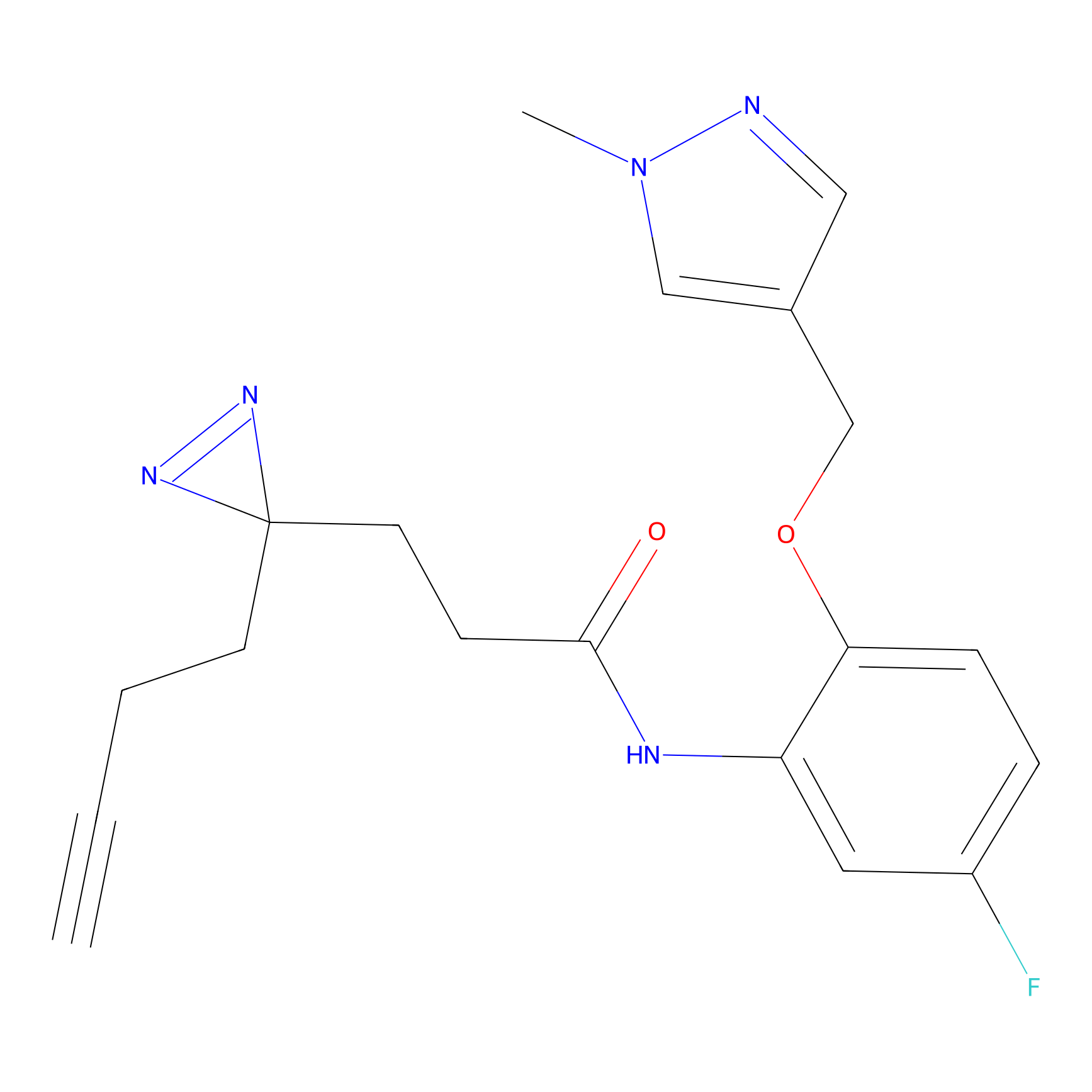
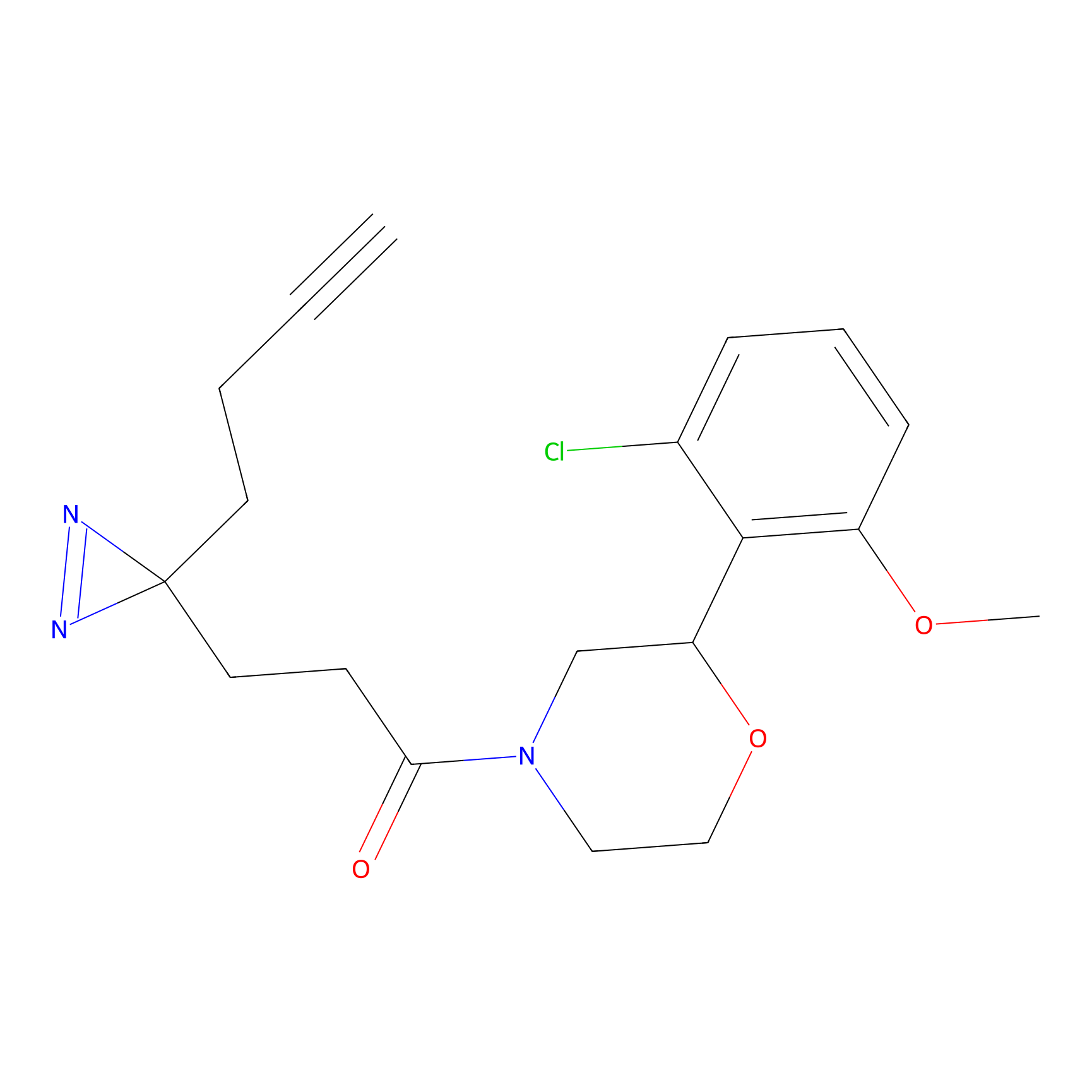
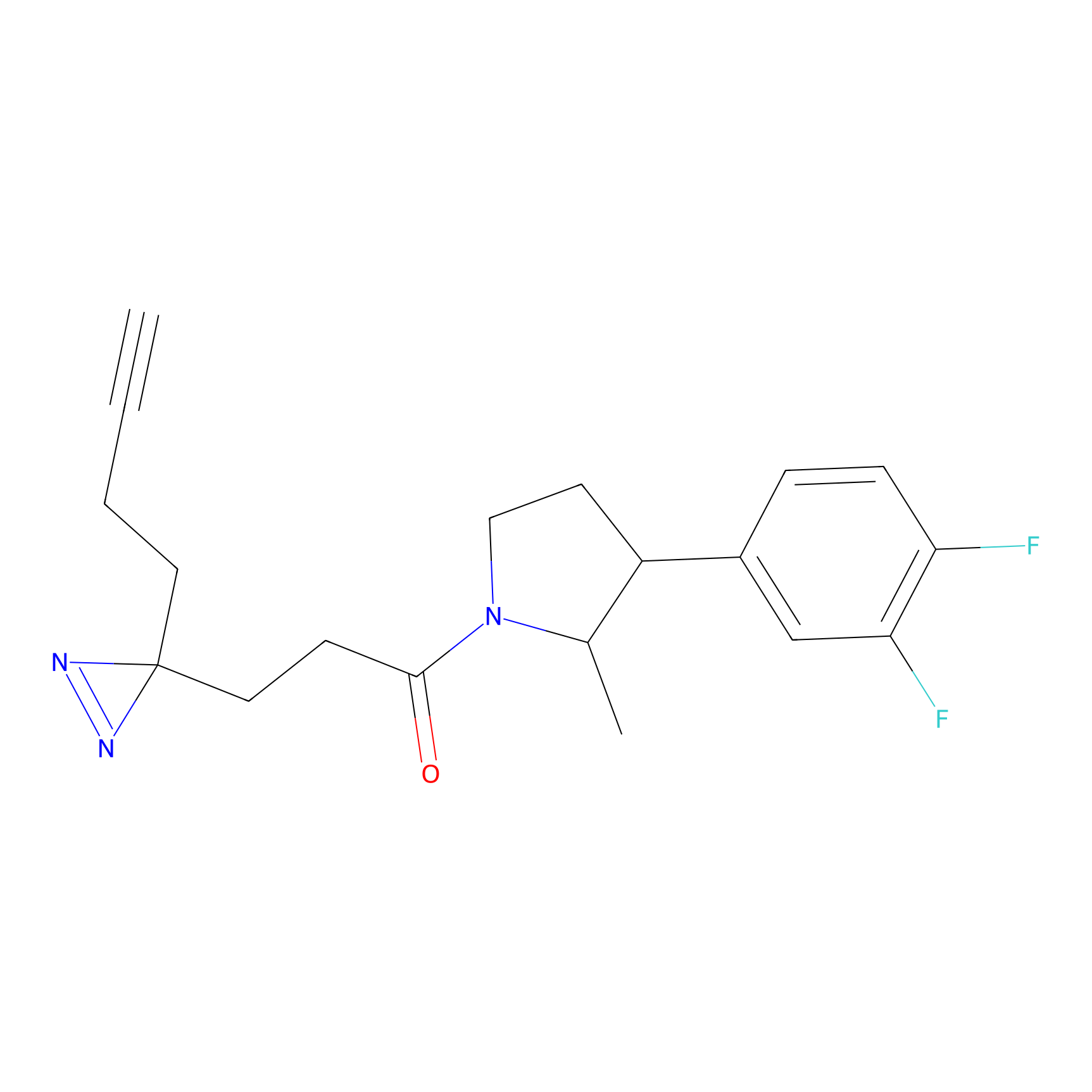
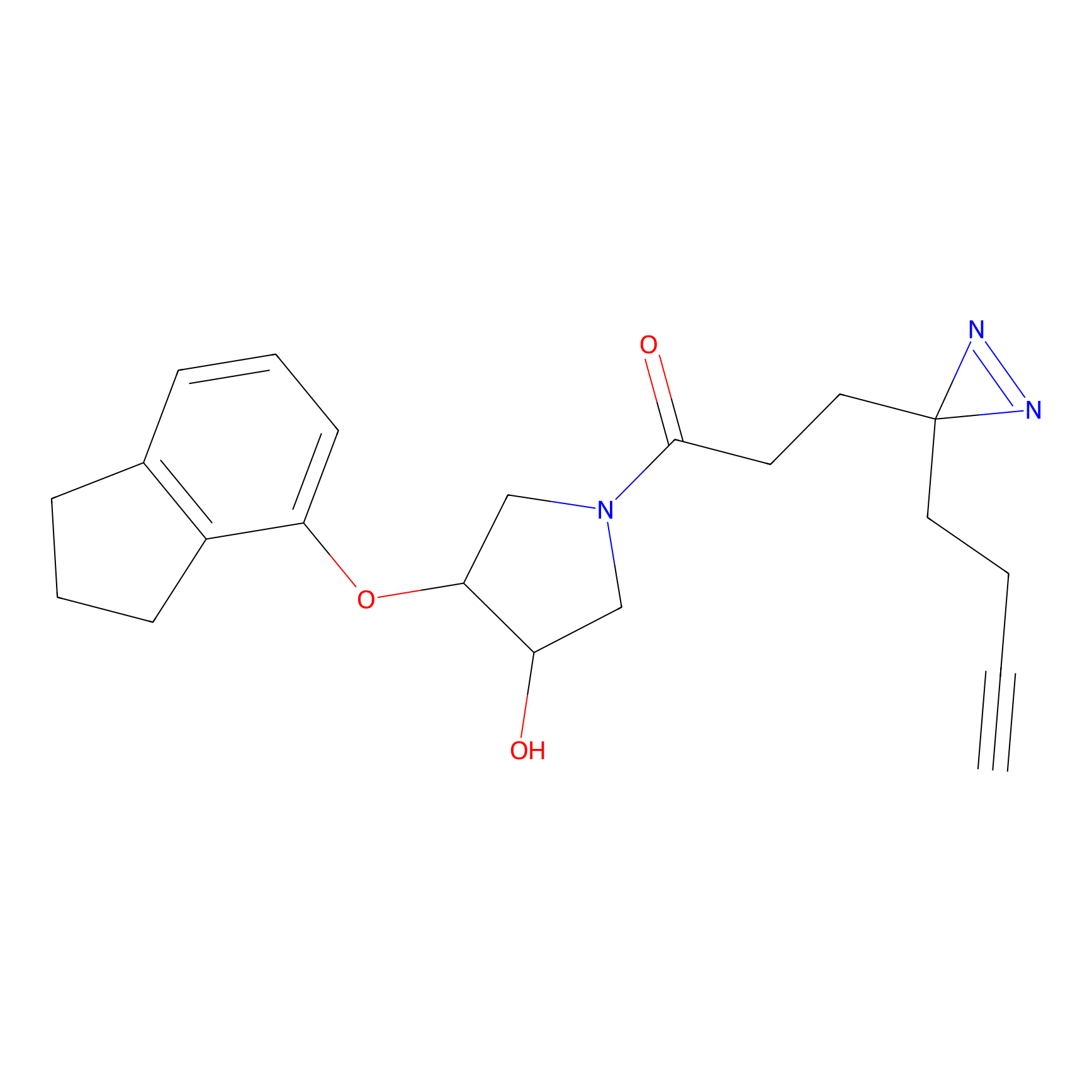
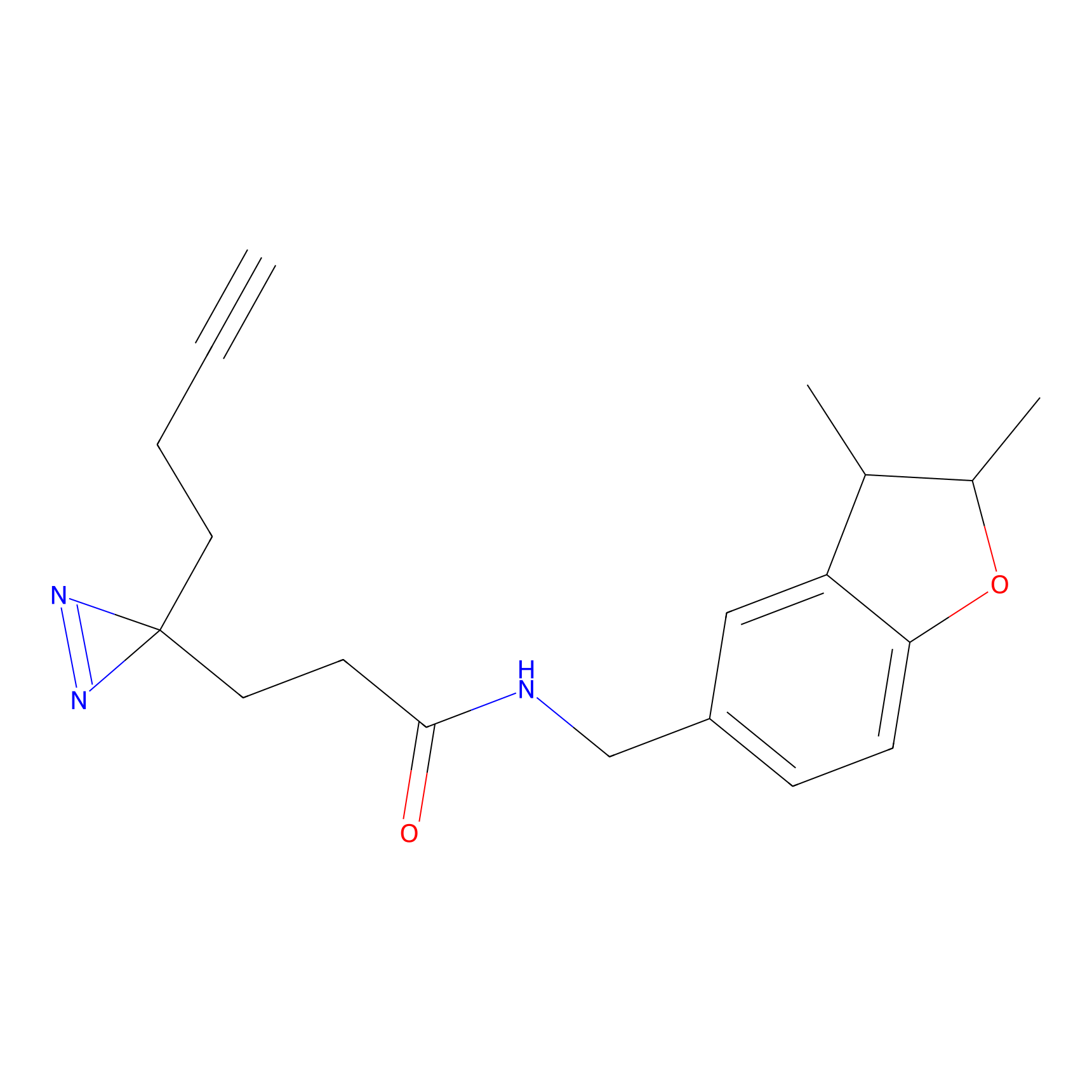
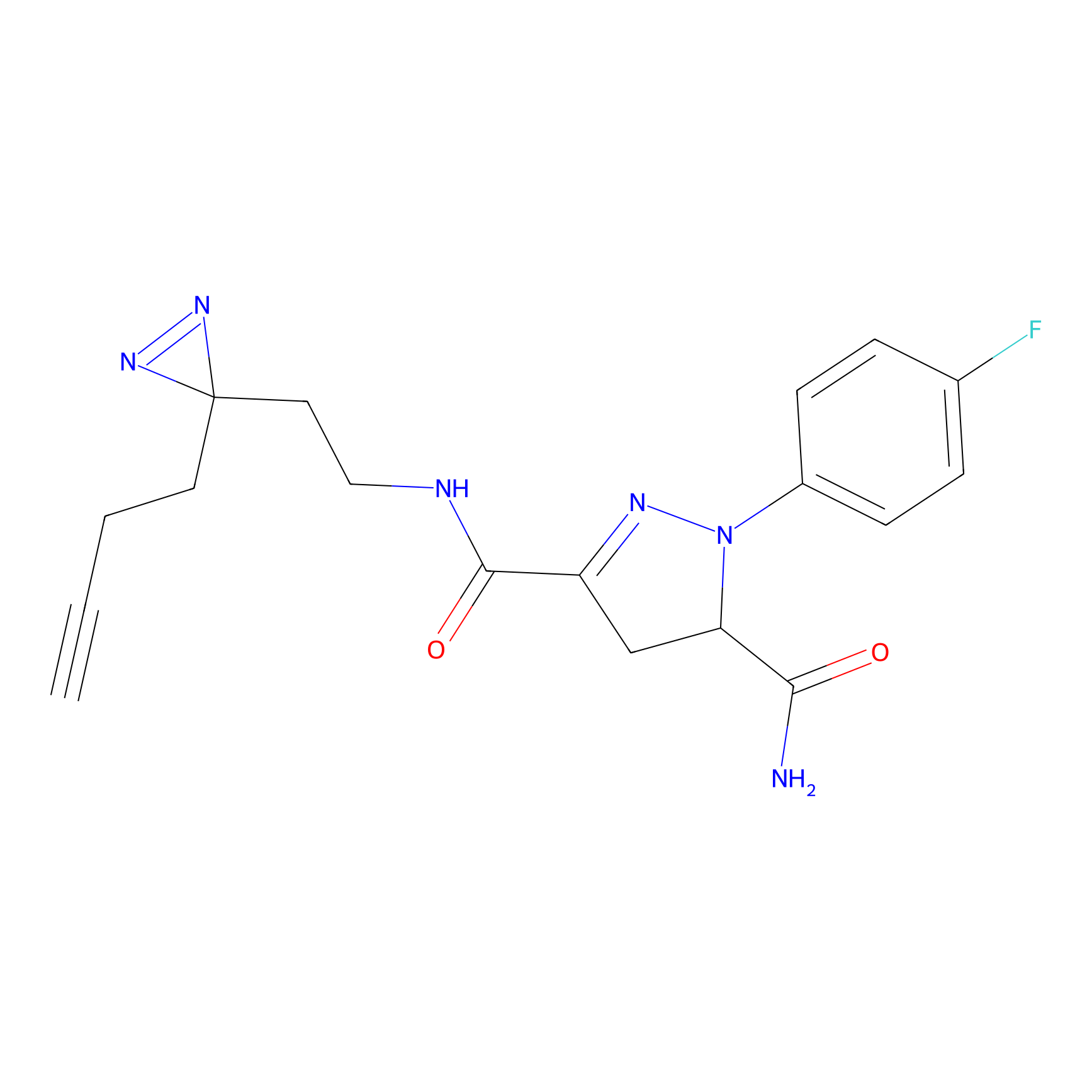
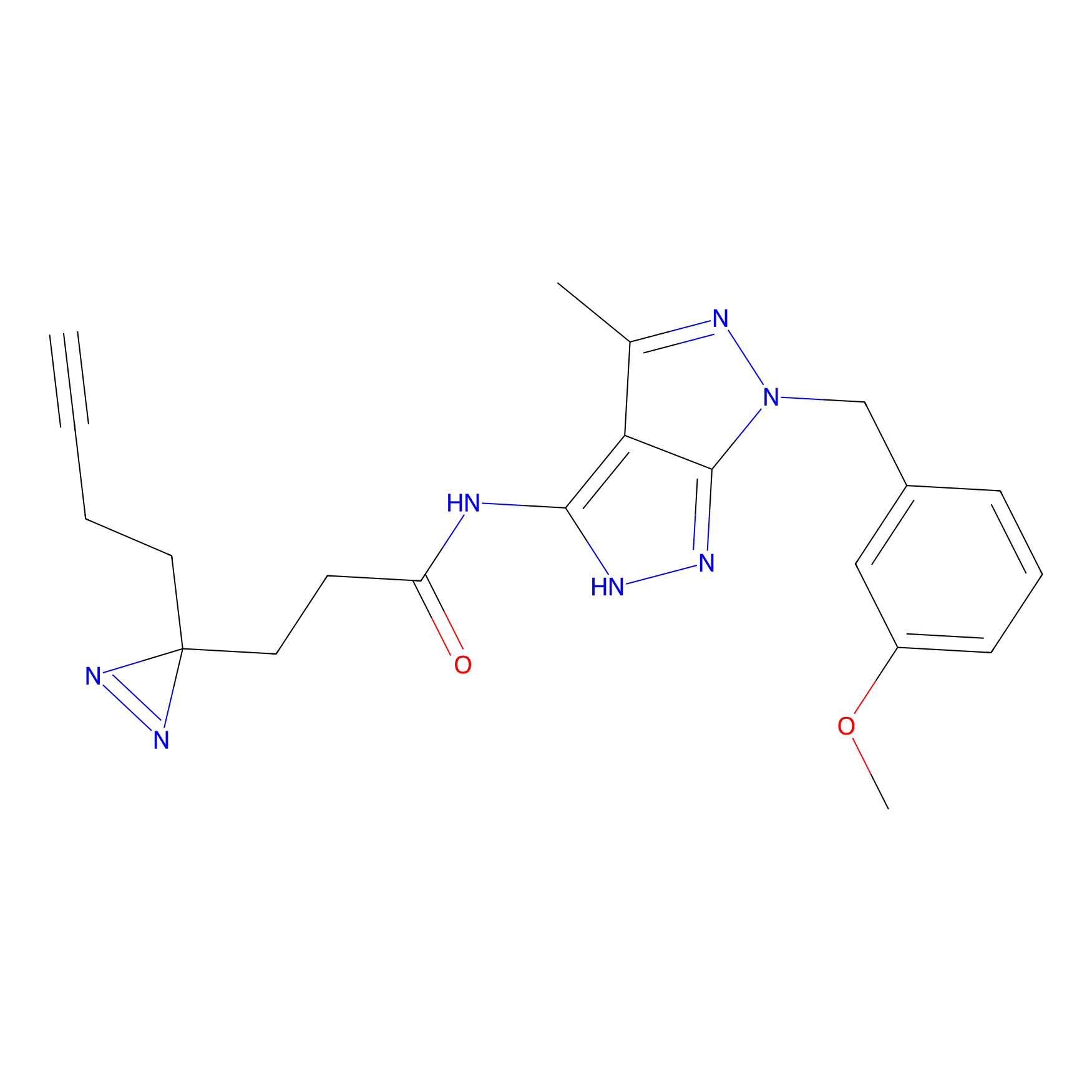
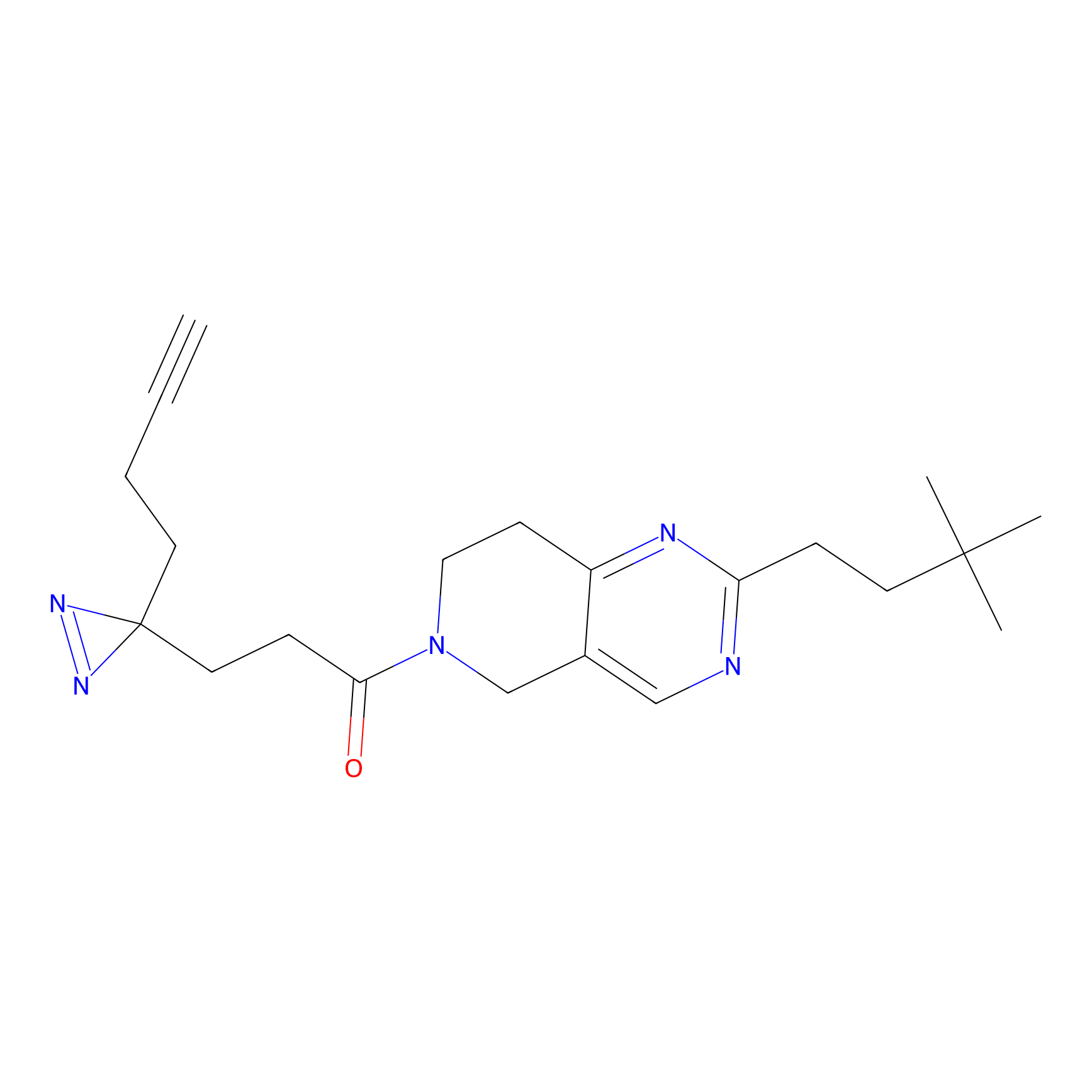
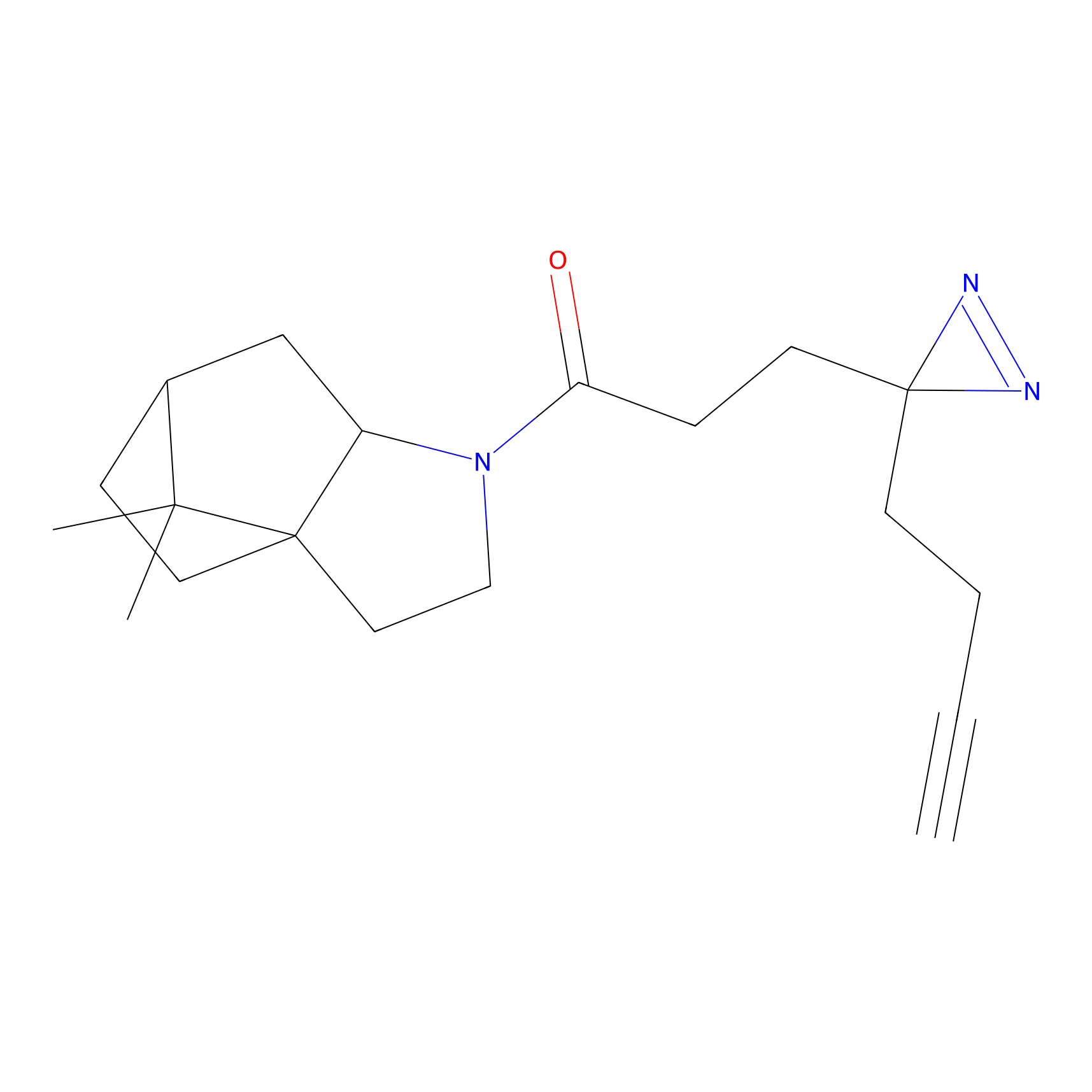
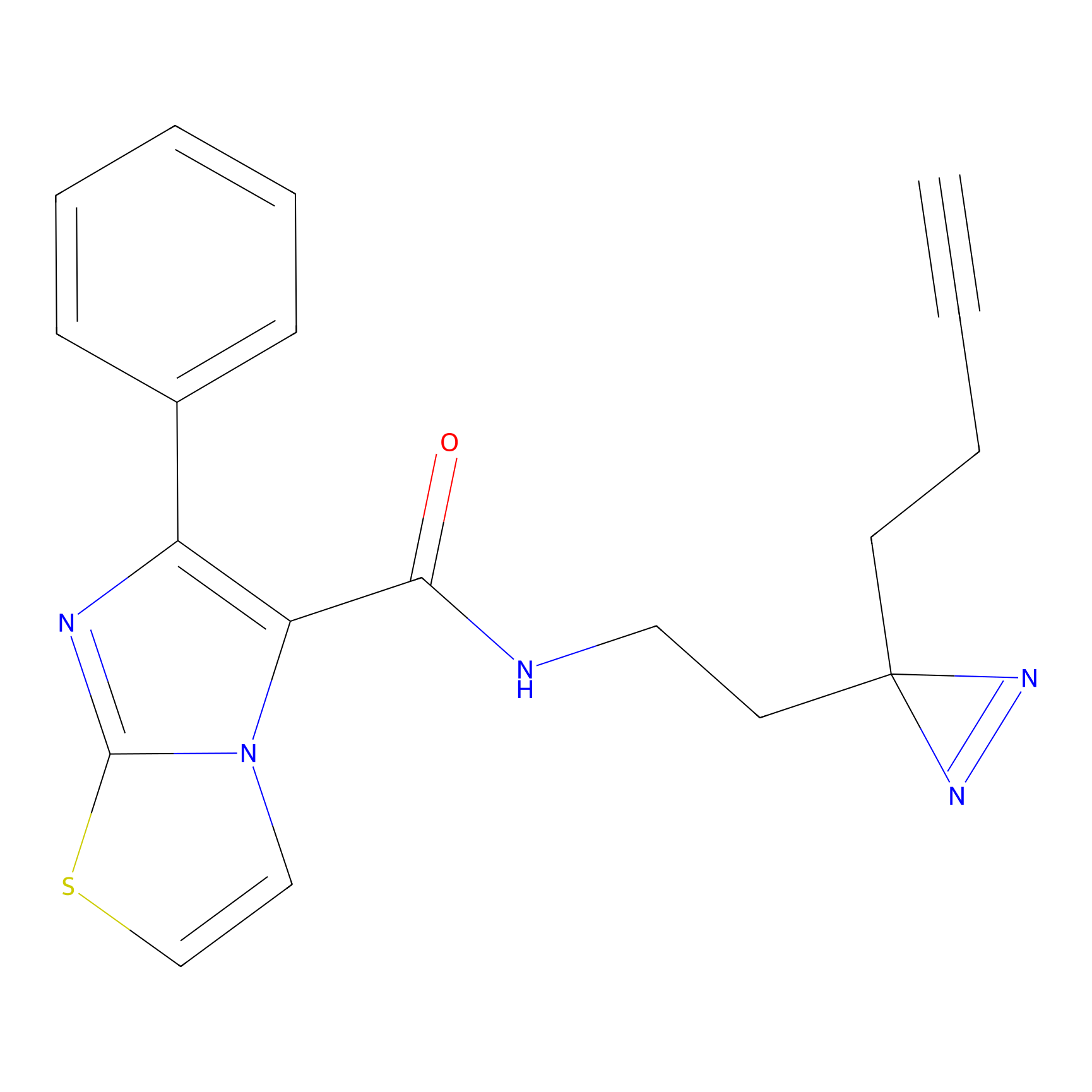
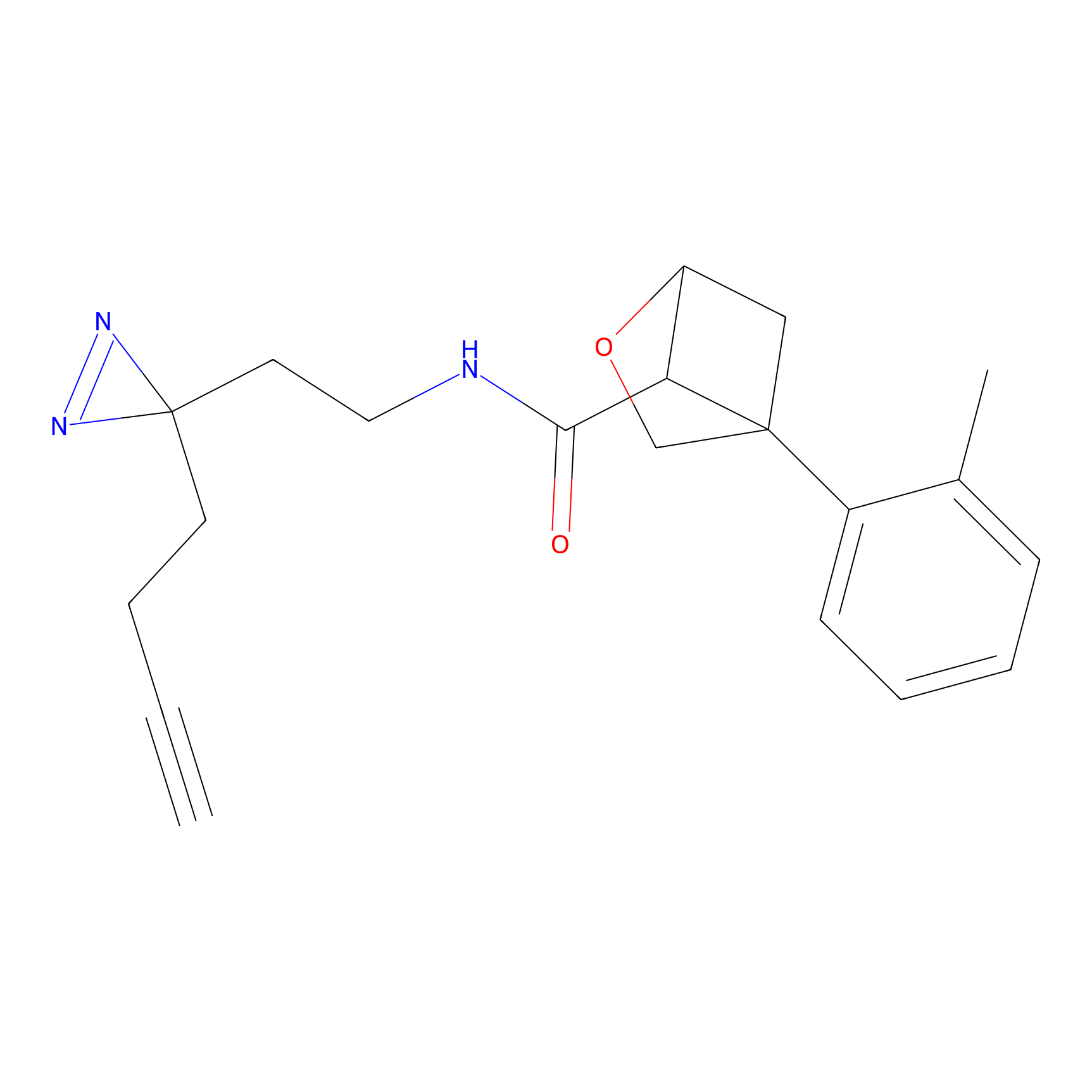
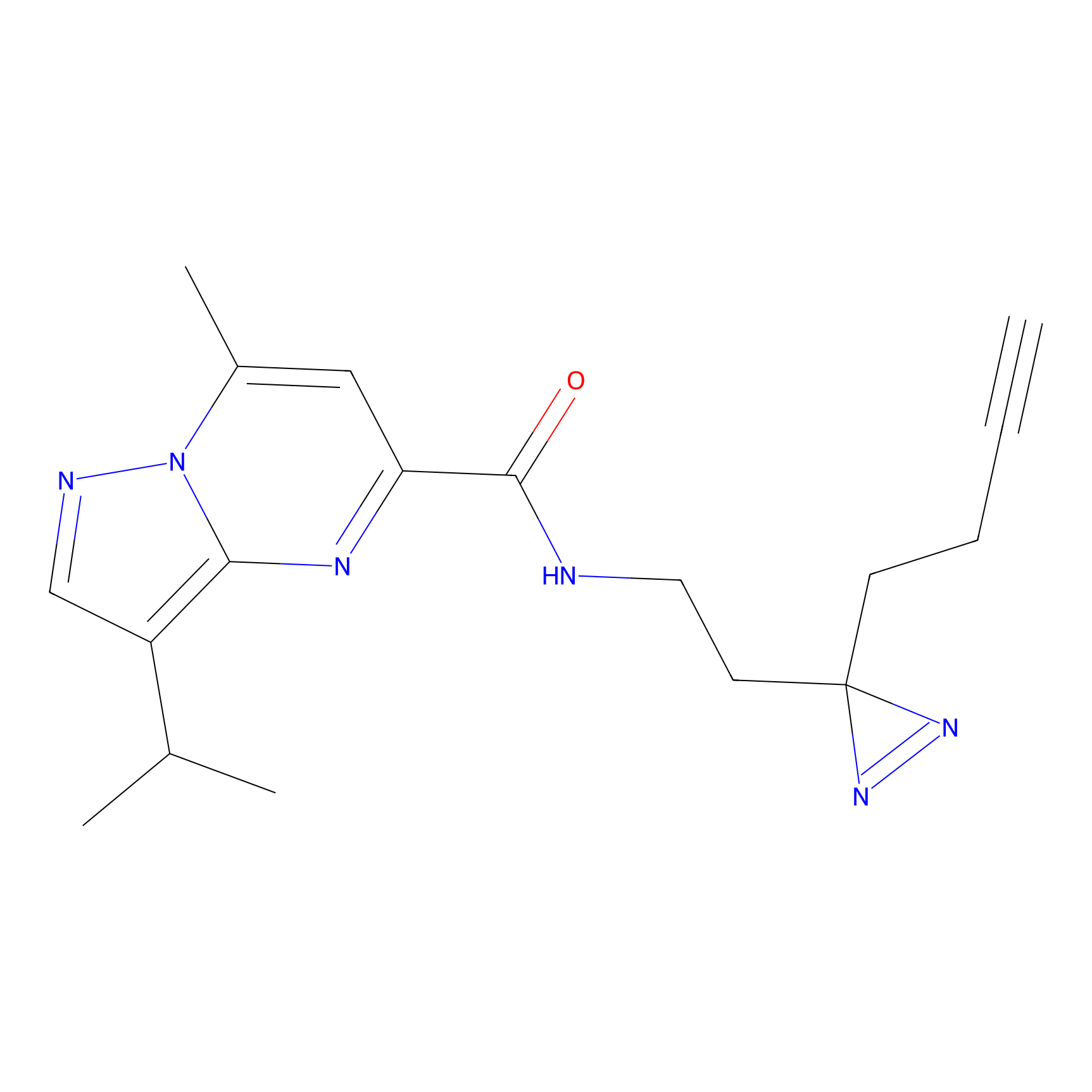
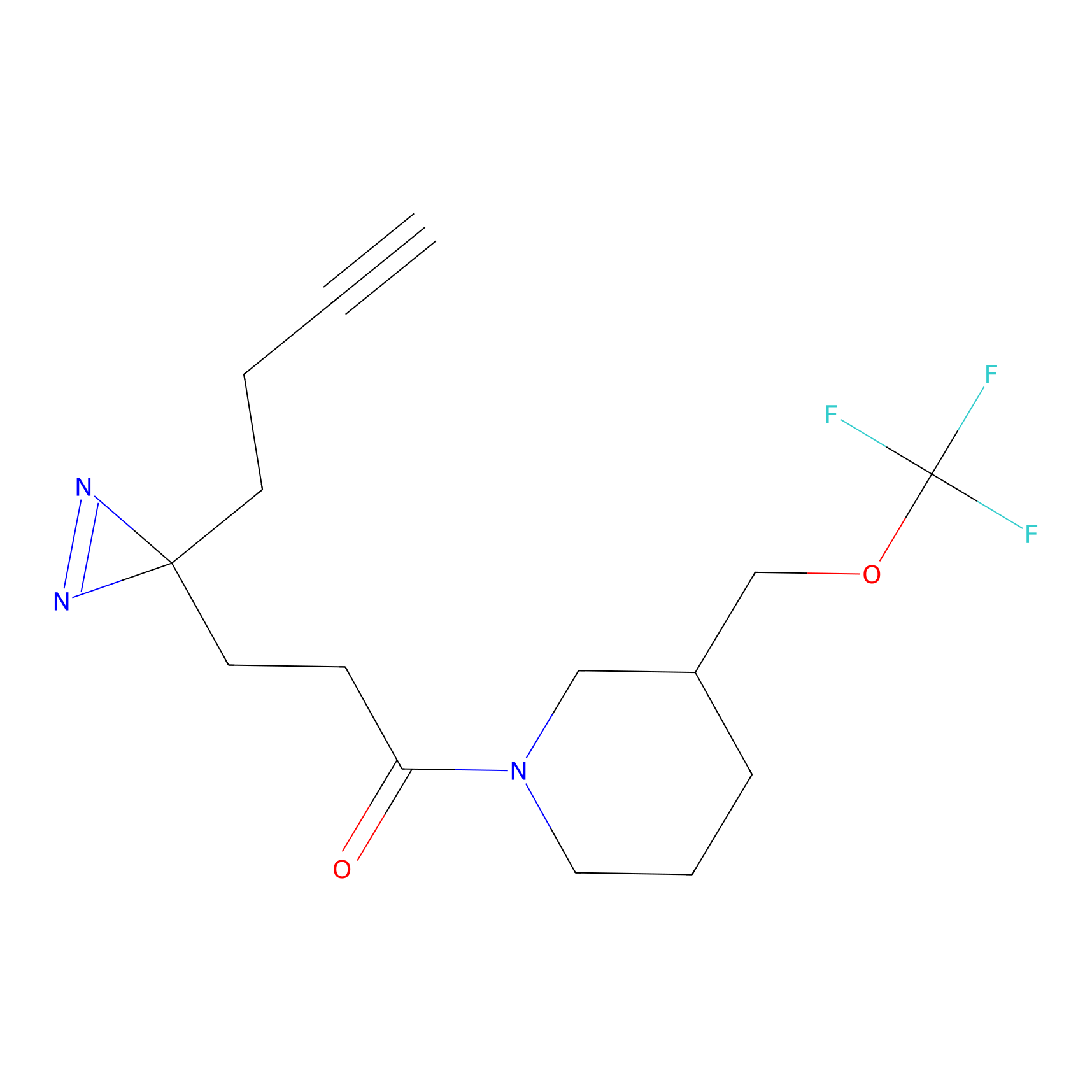
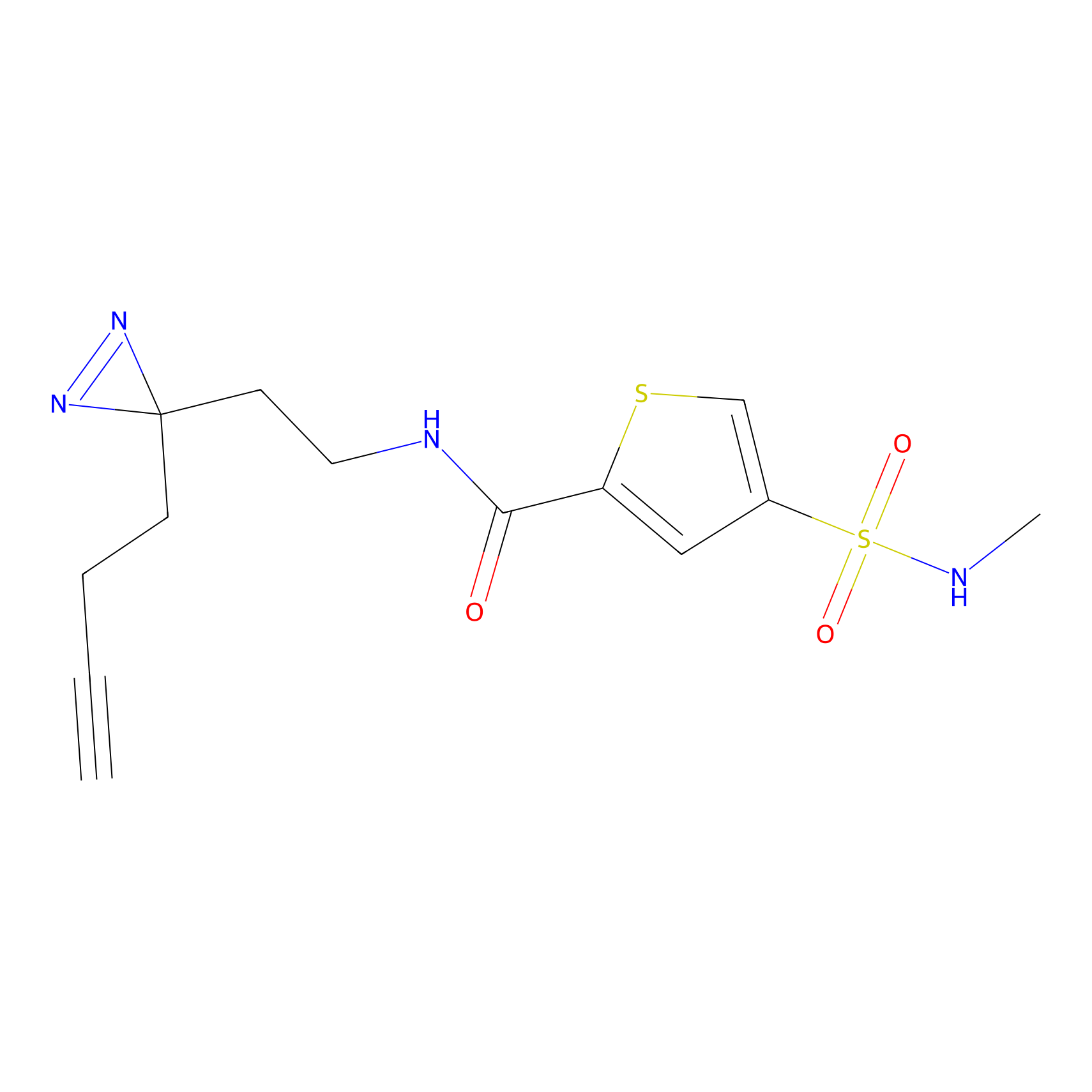
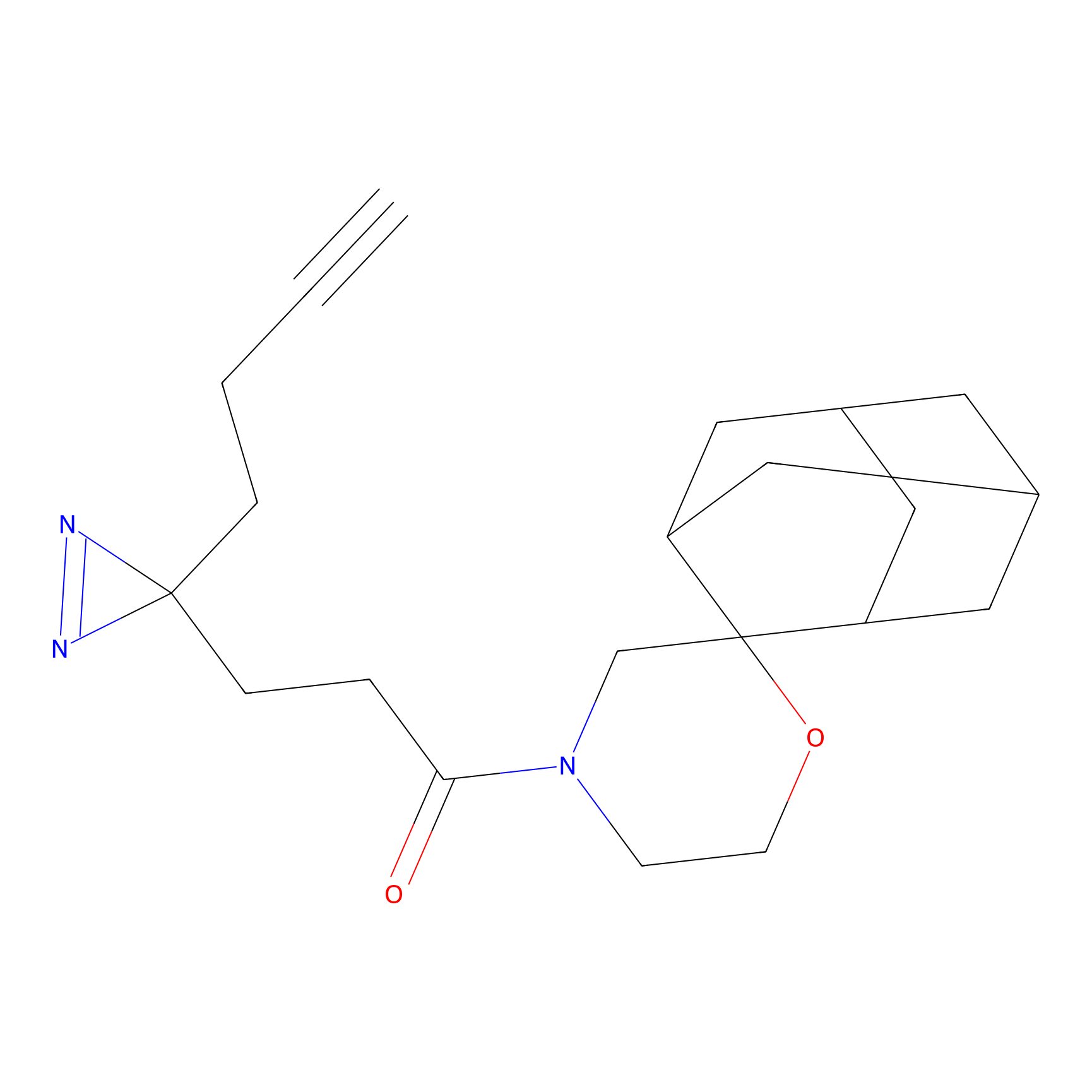
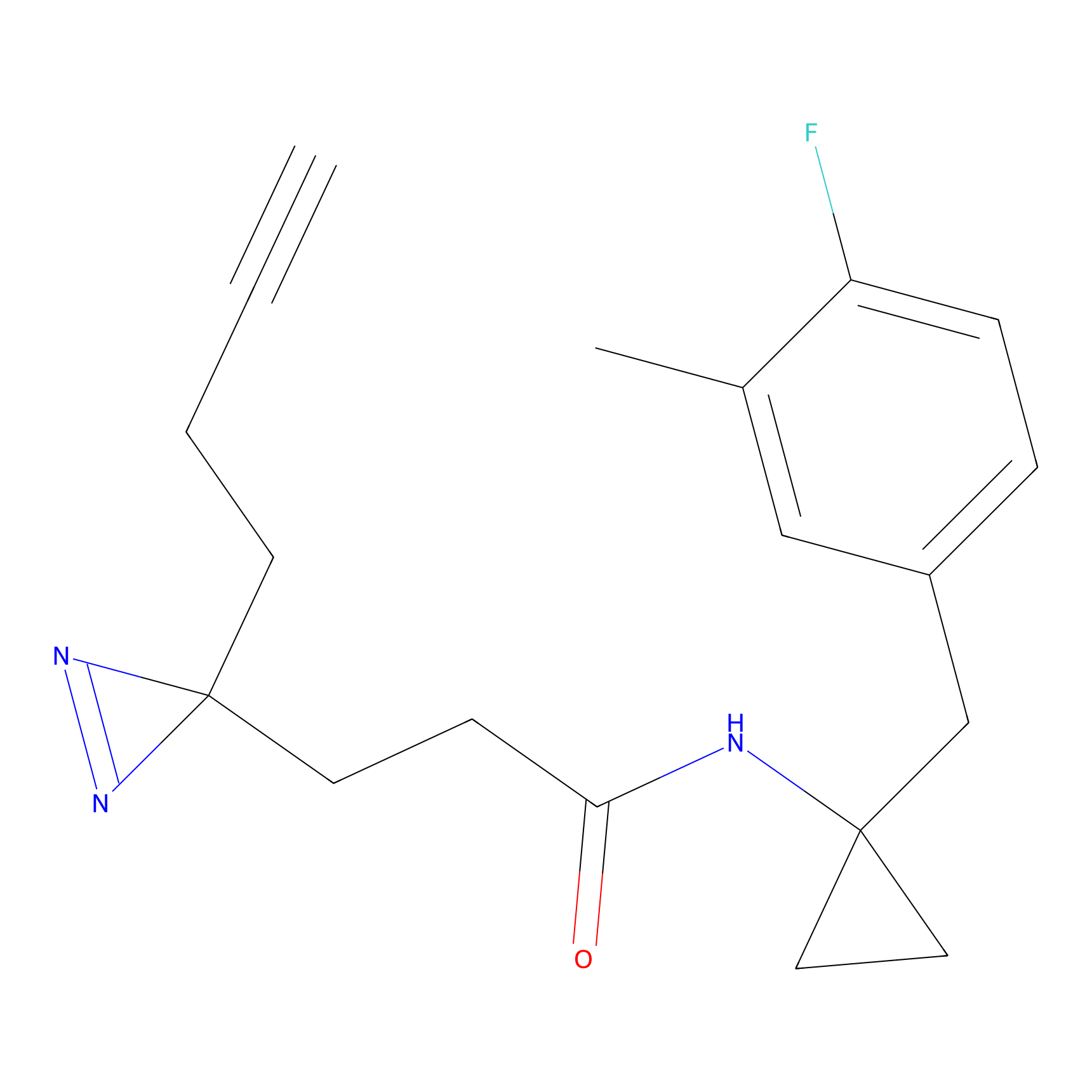
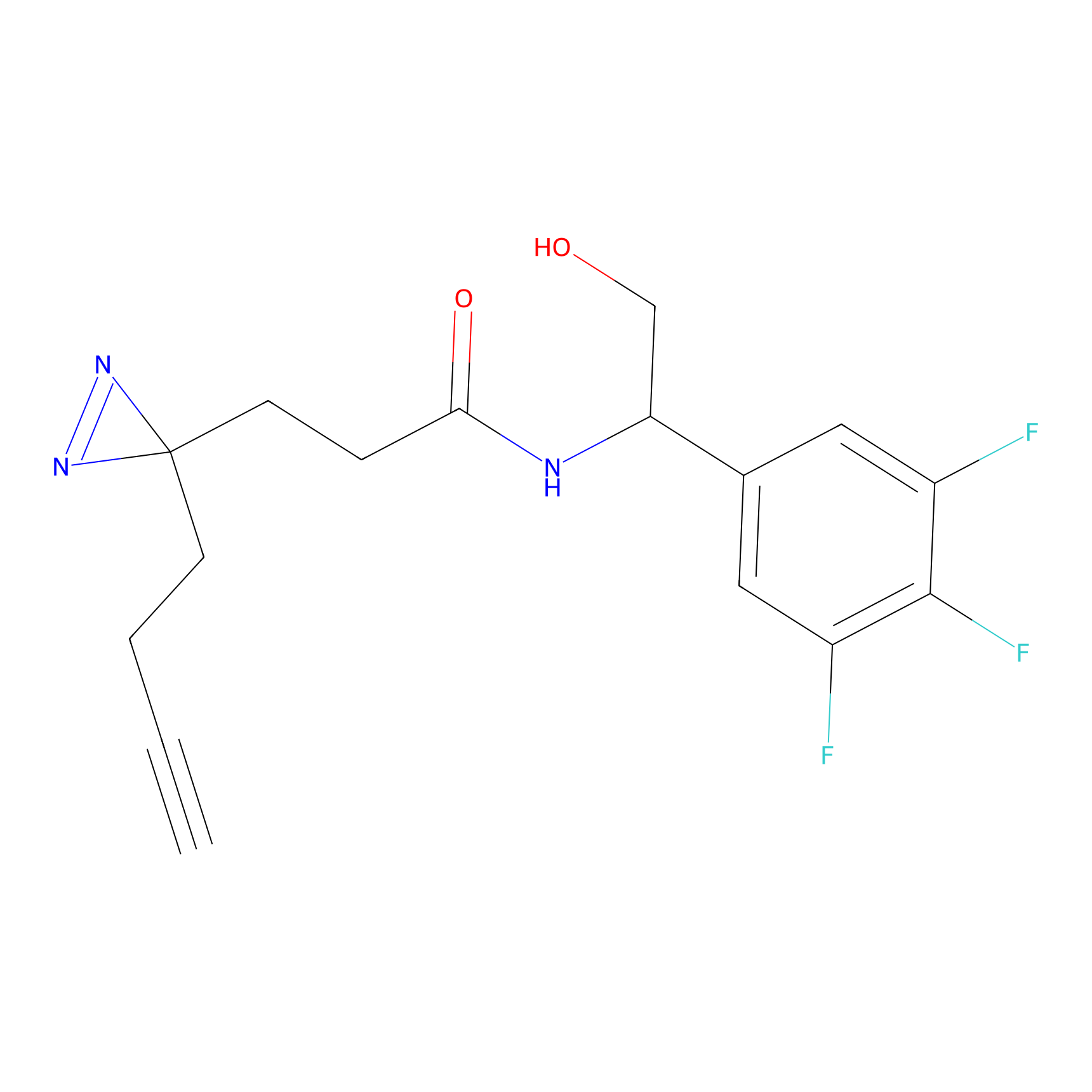
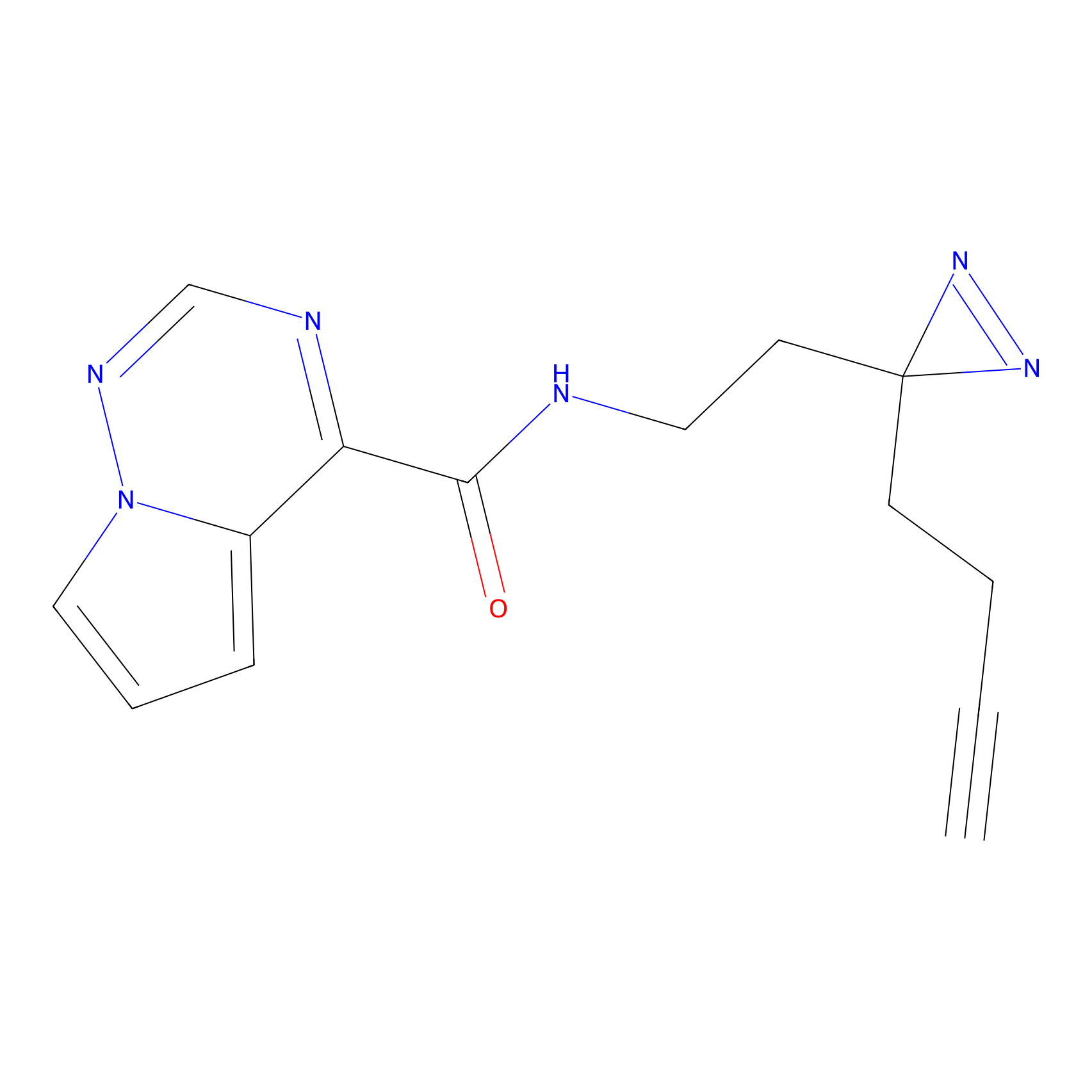
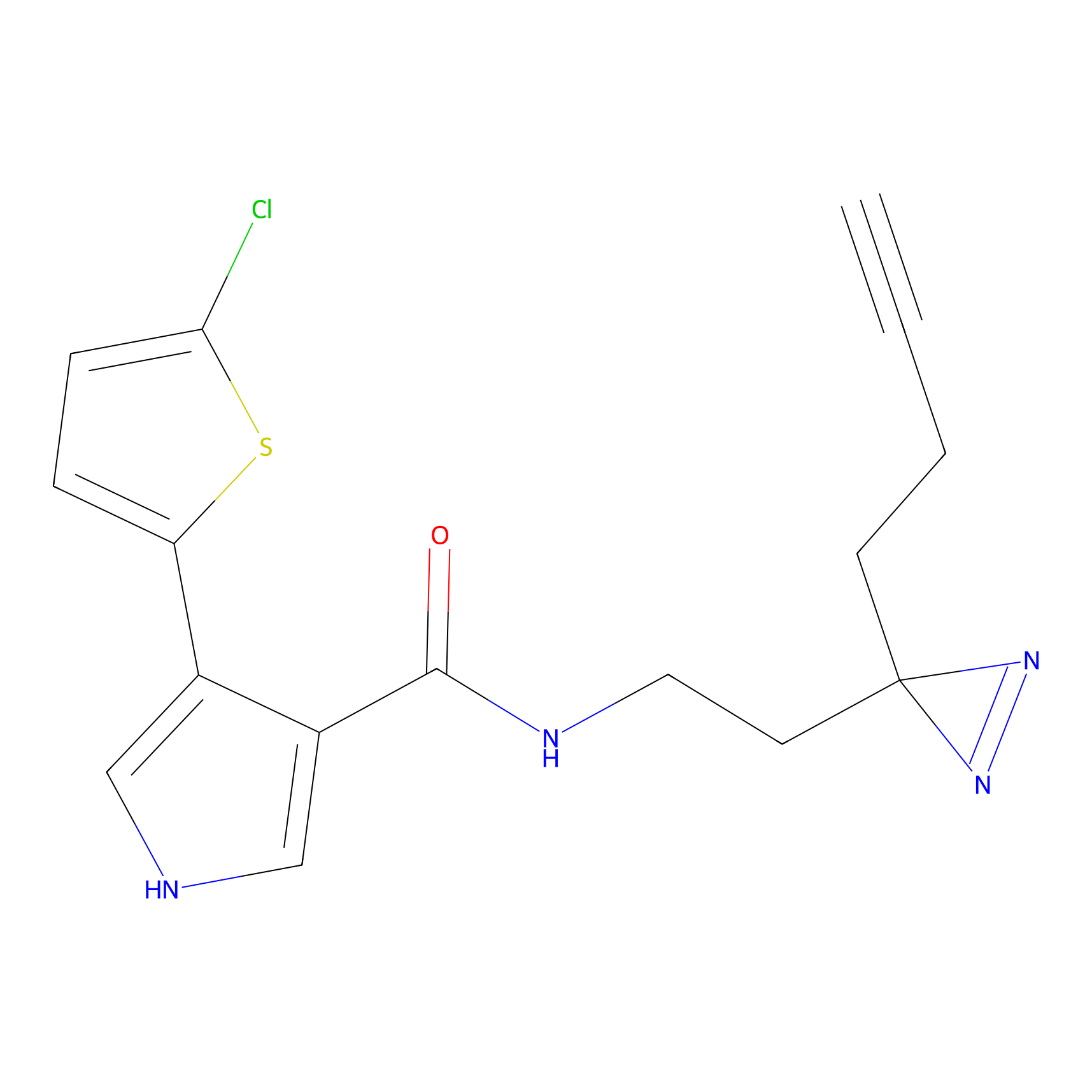
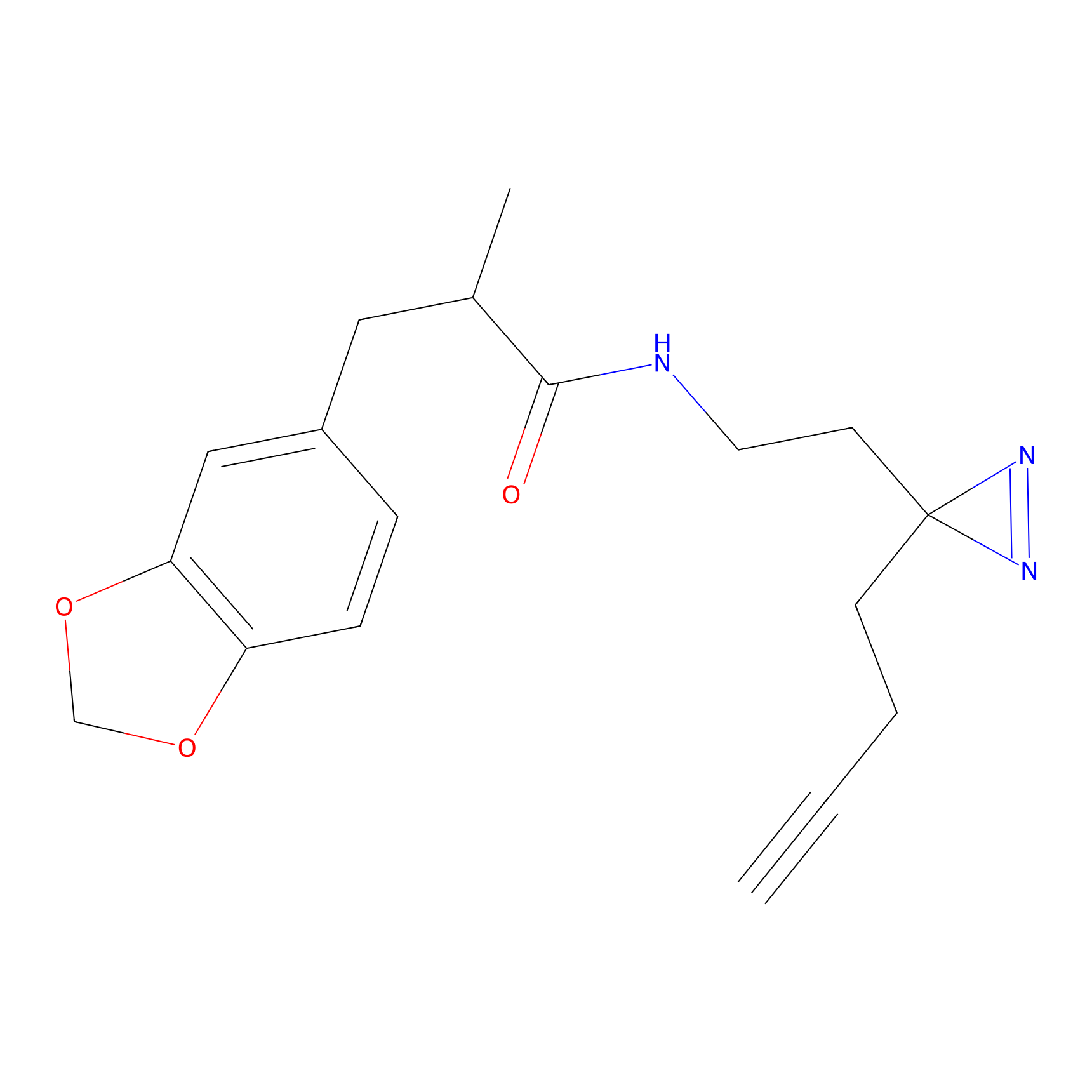
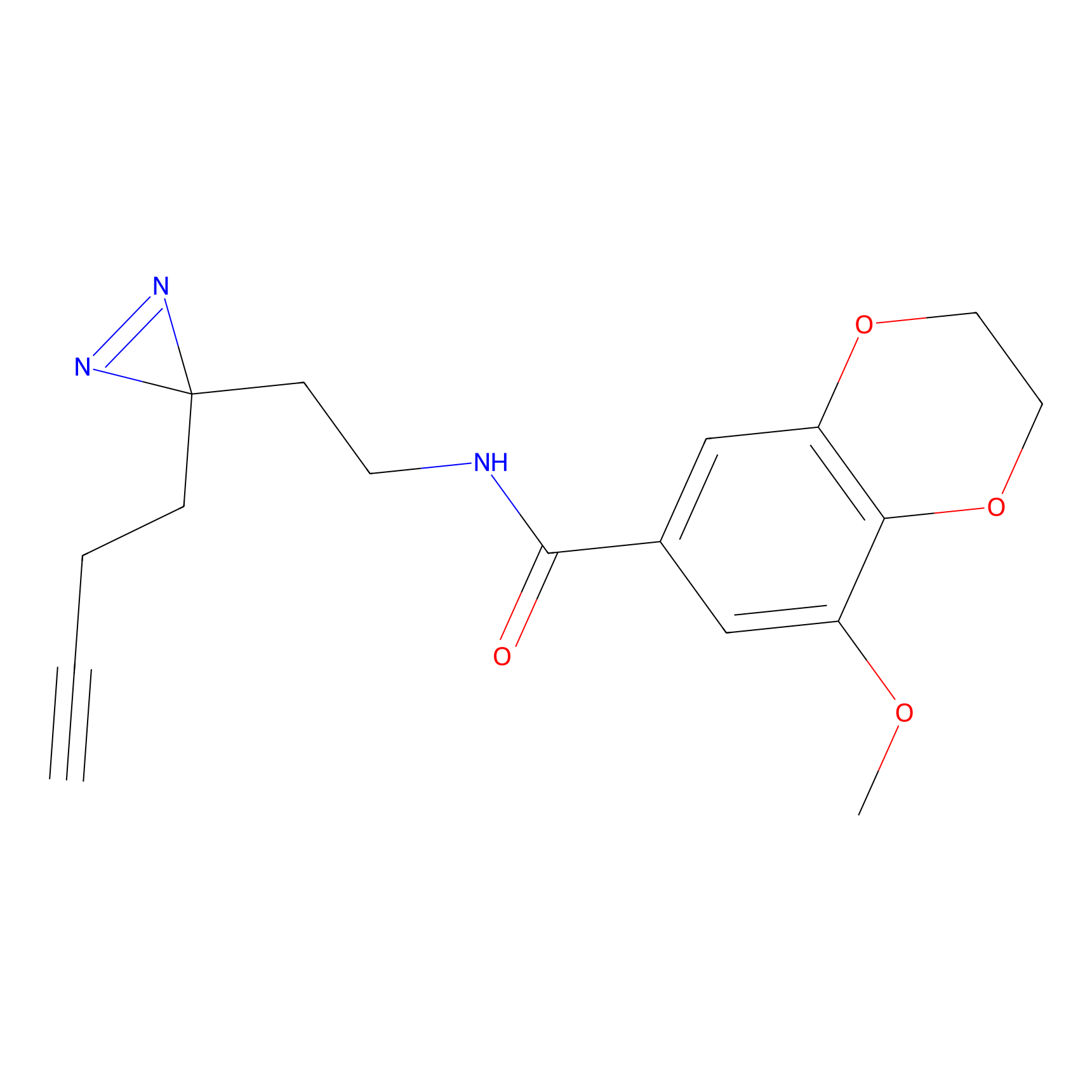
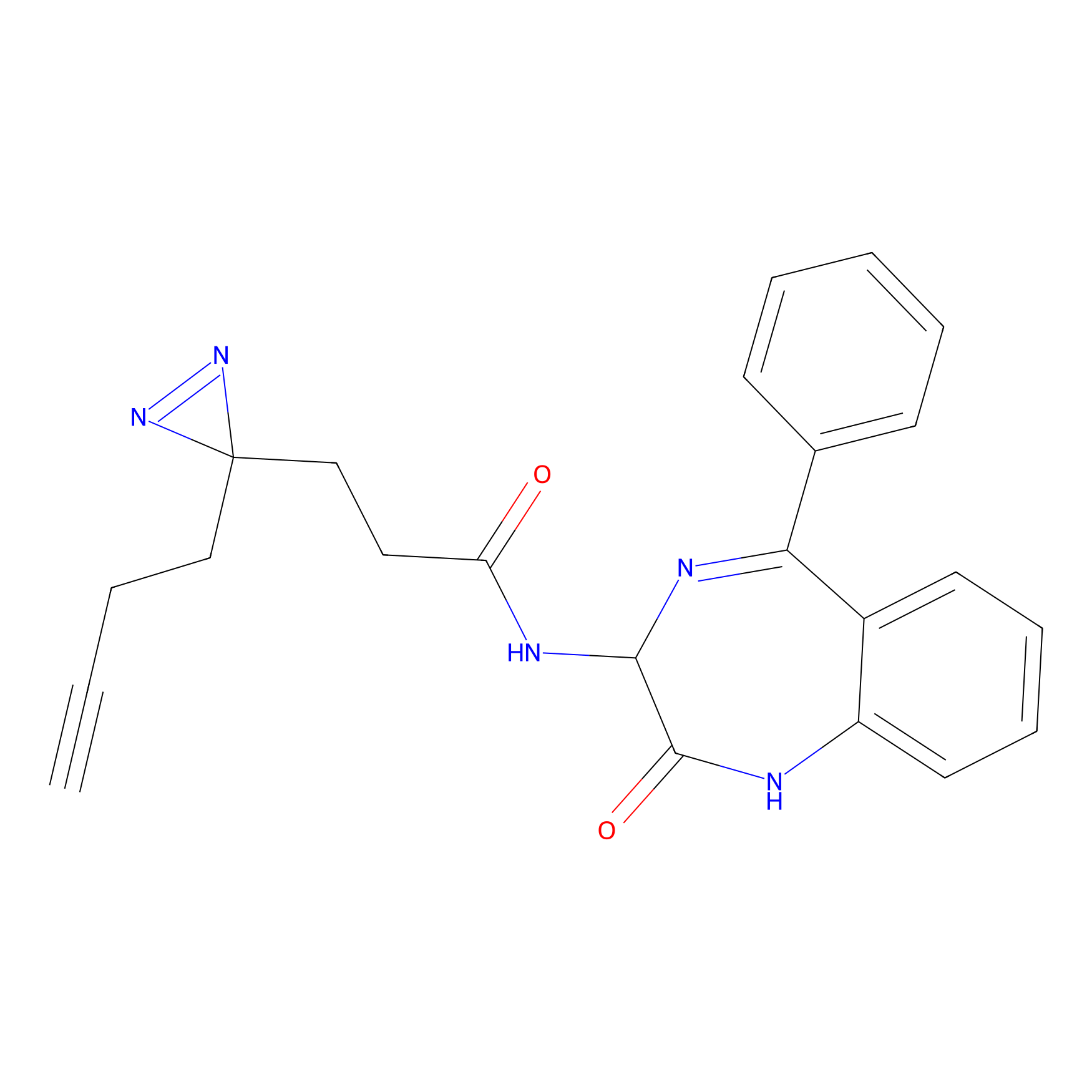
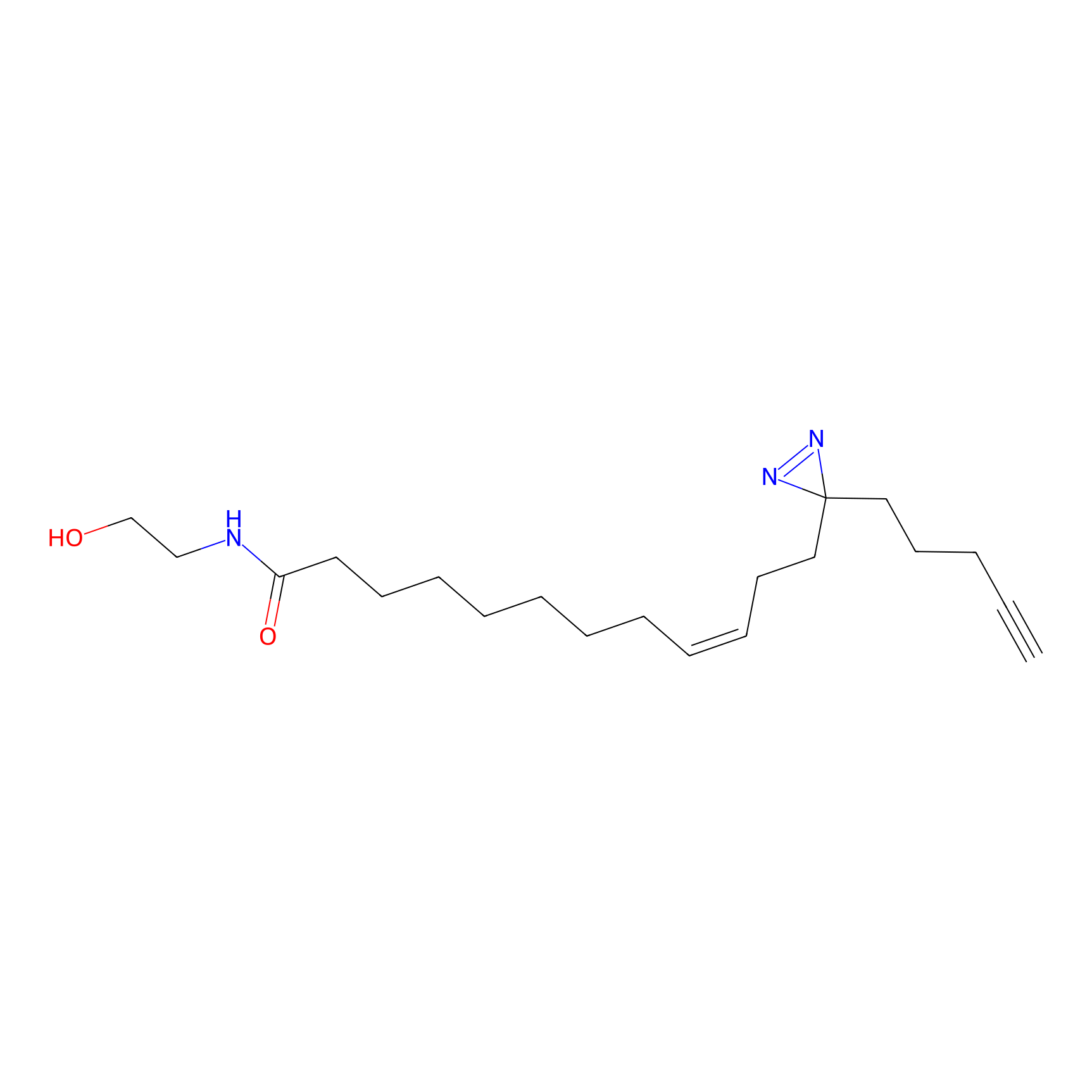
|
Acrolein Probe Info |
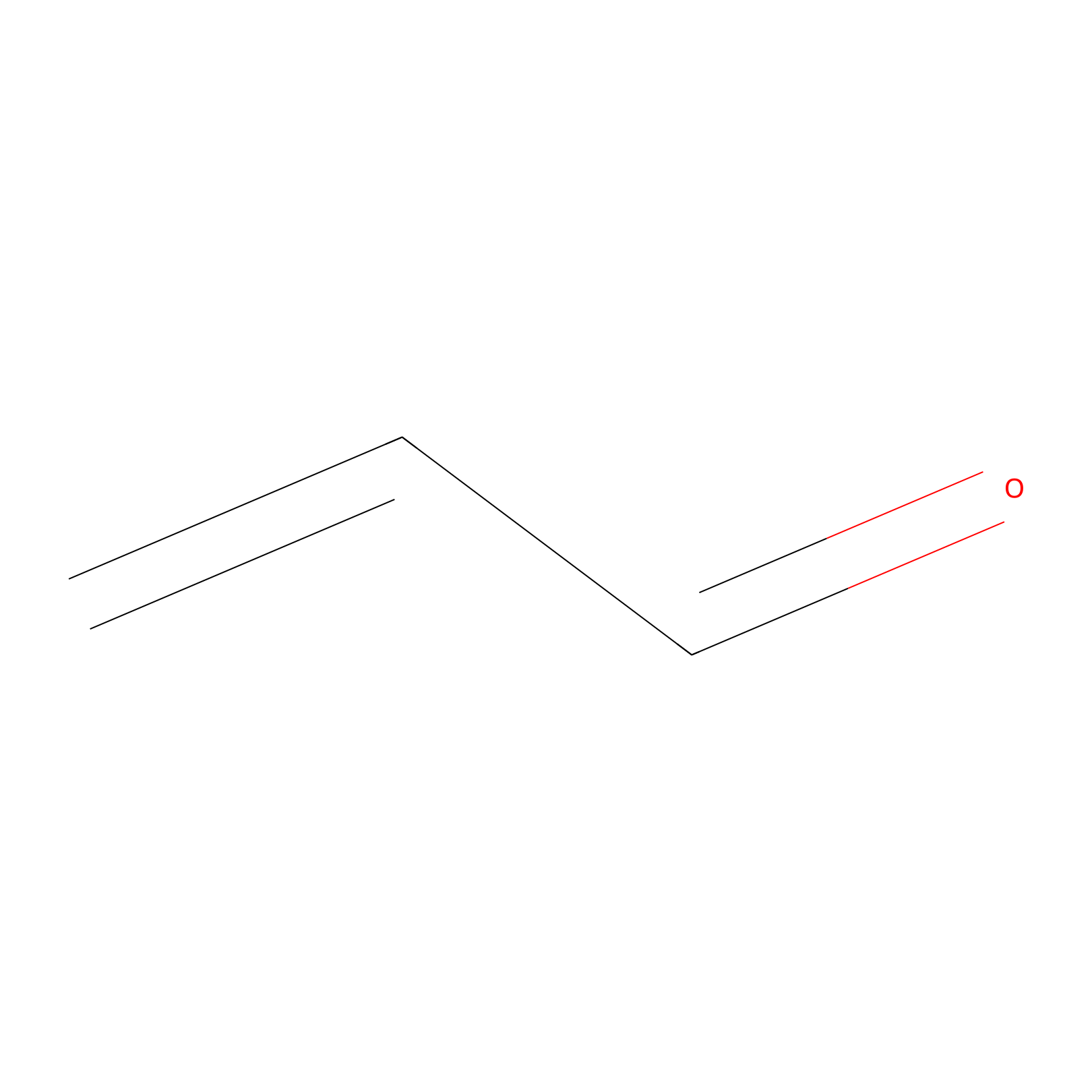 |
N.A. | LDD0217 | [2] | |
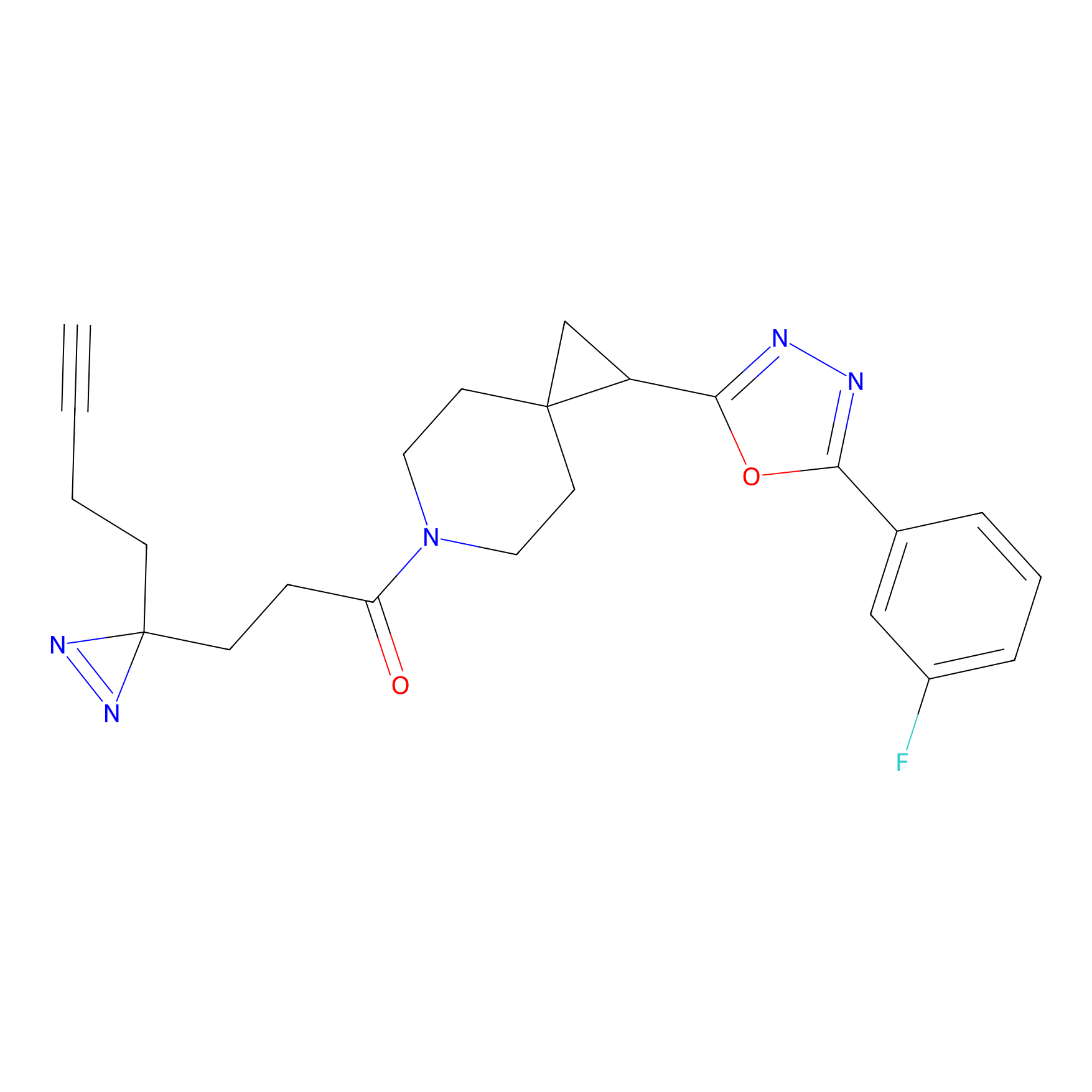
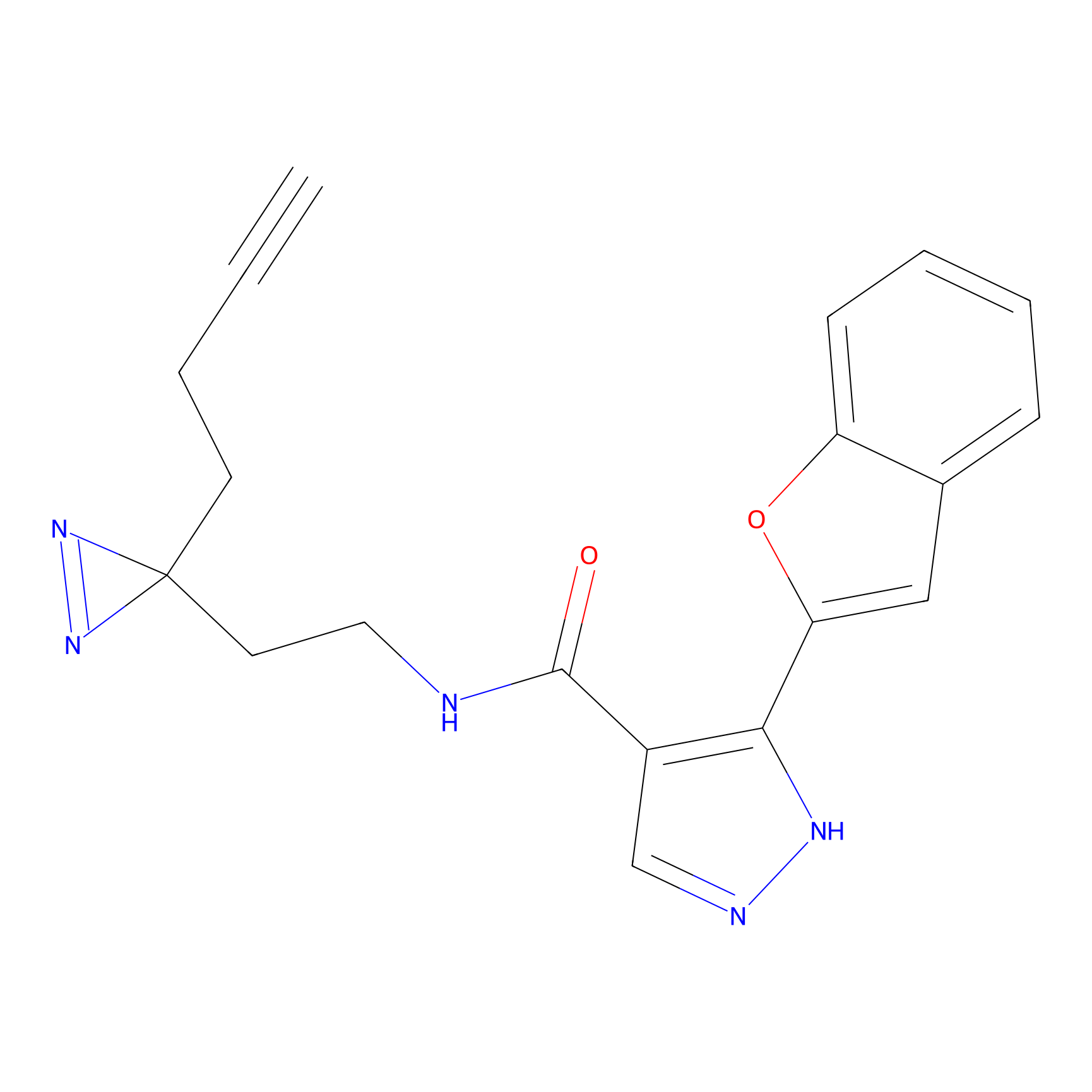
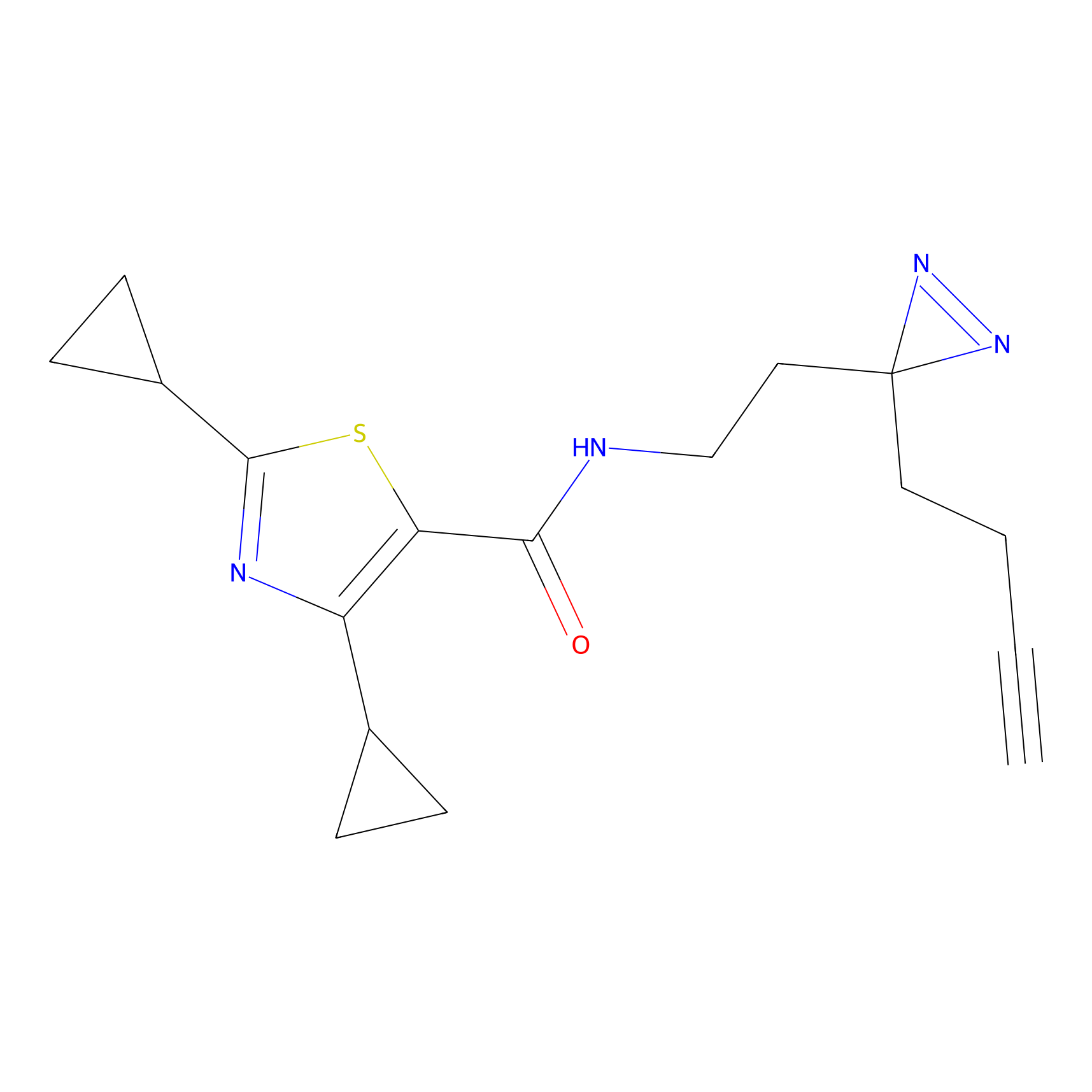
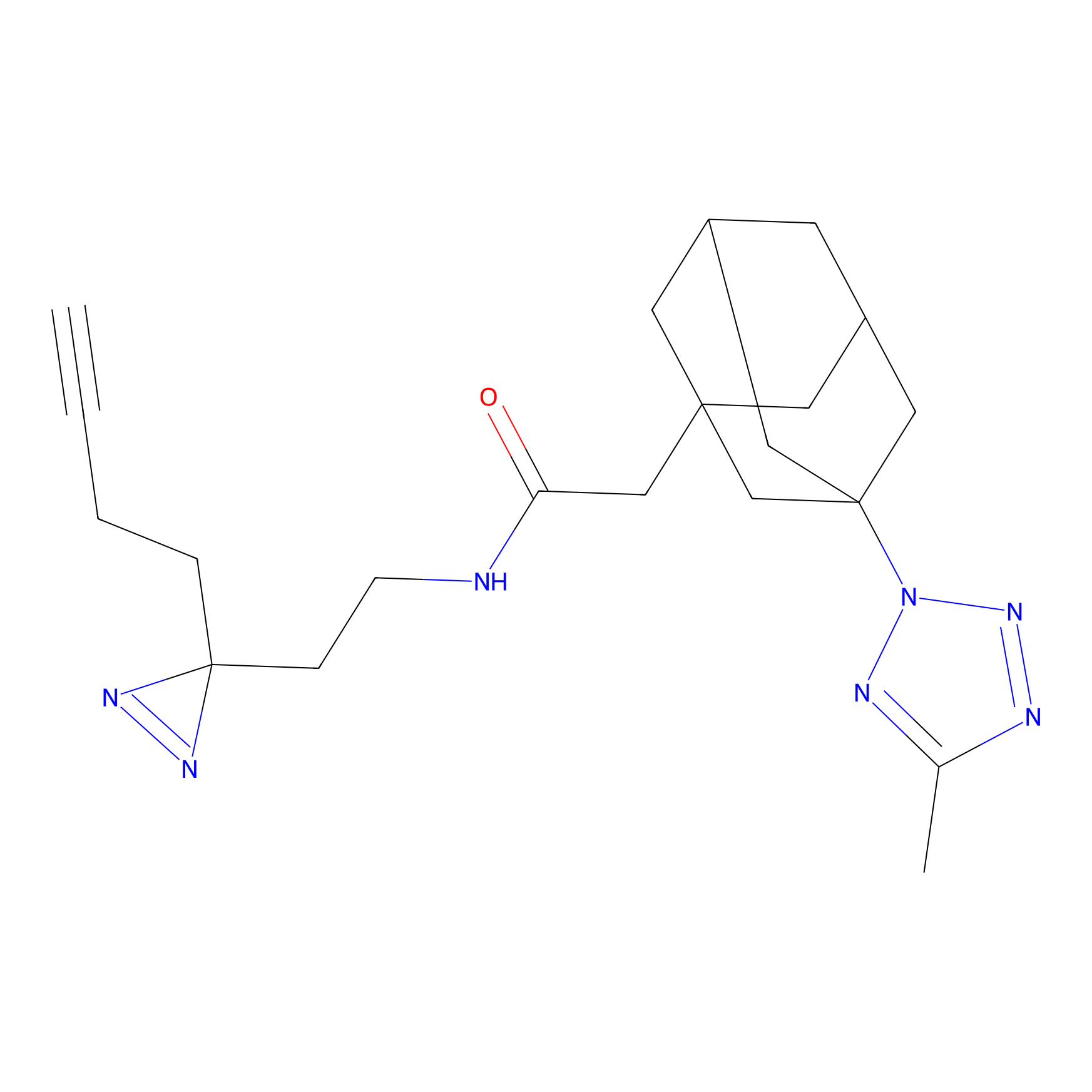
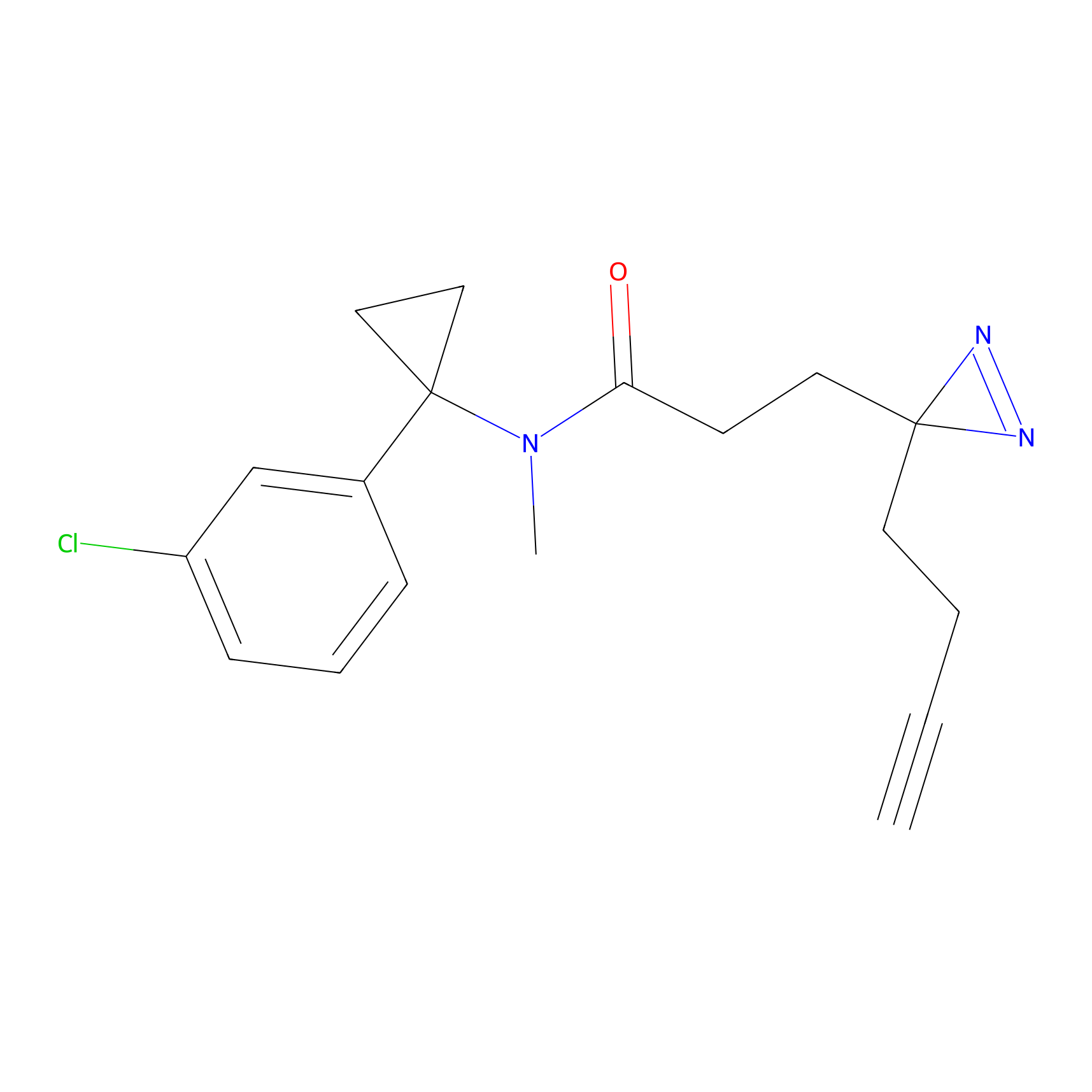
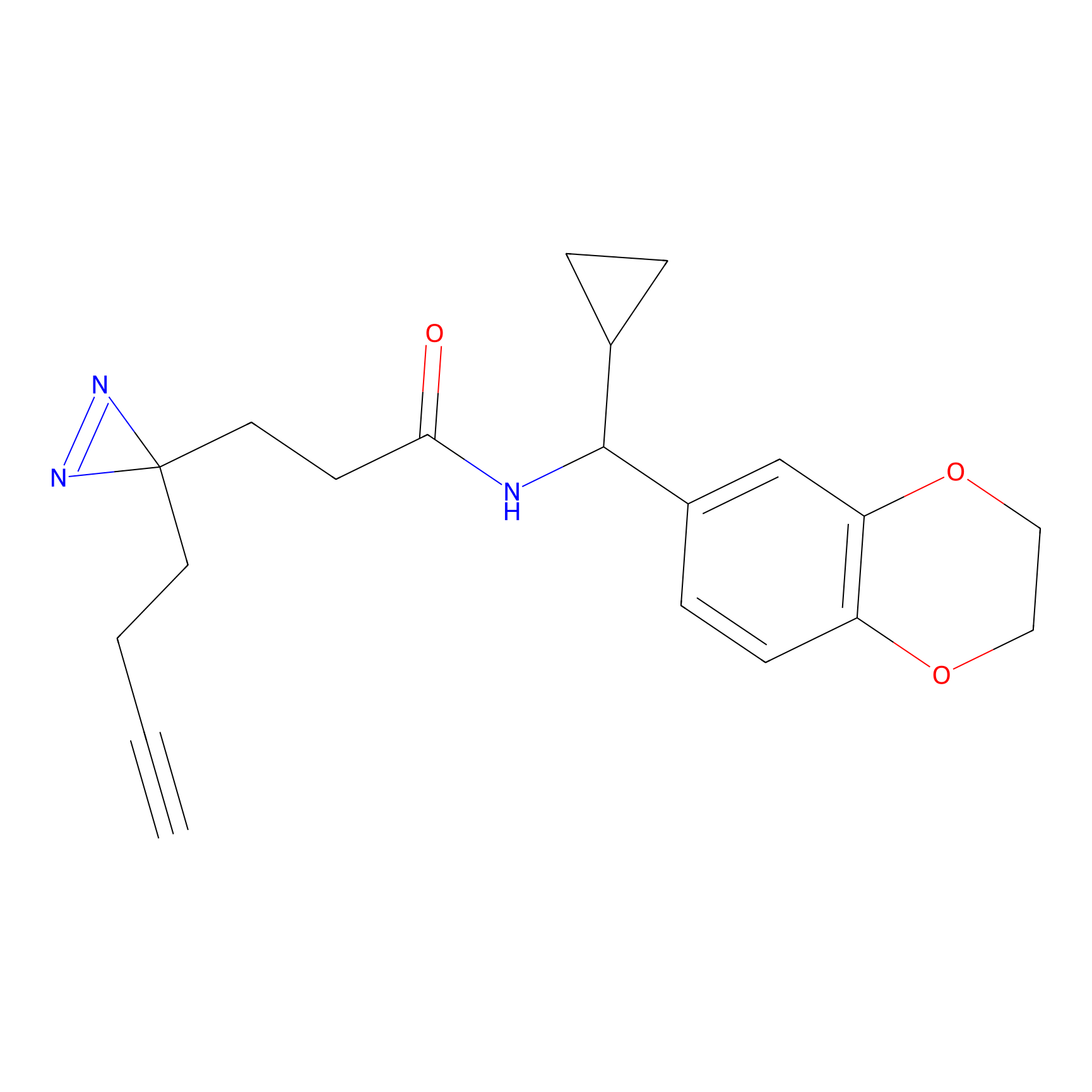
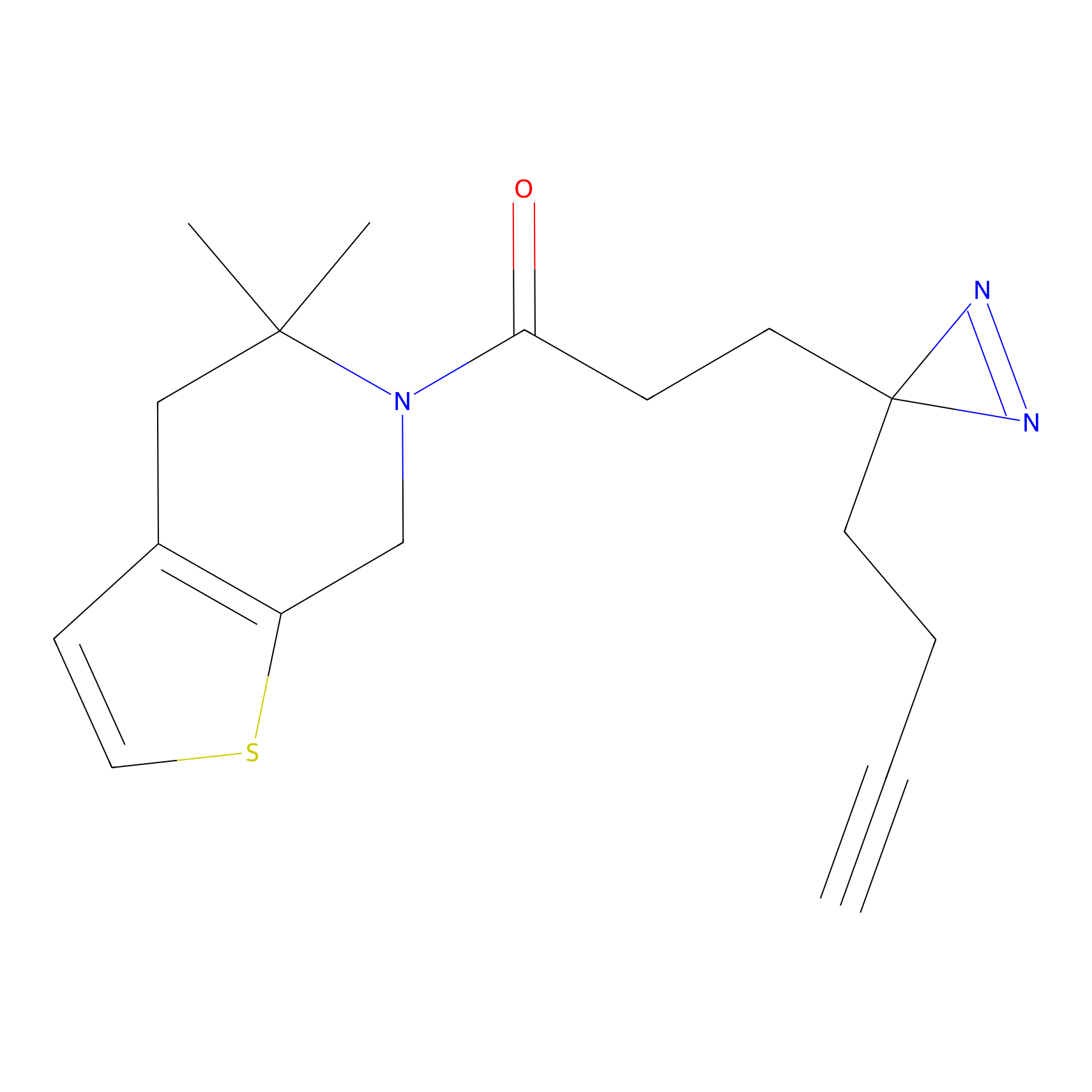
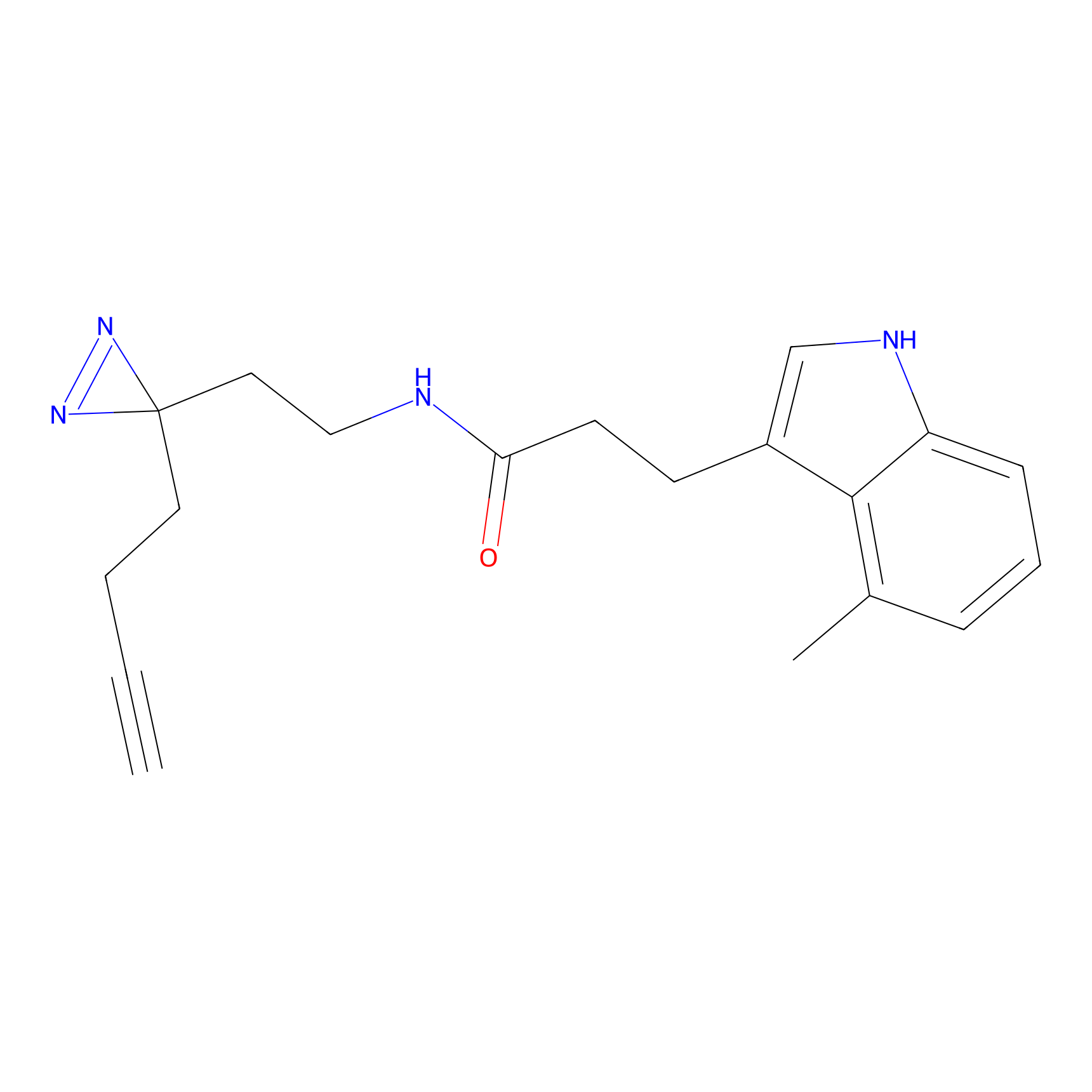
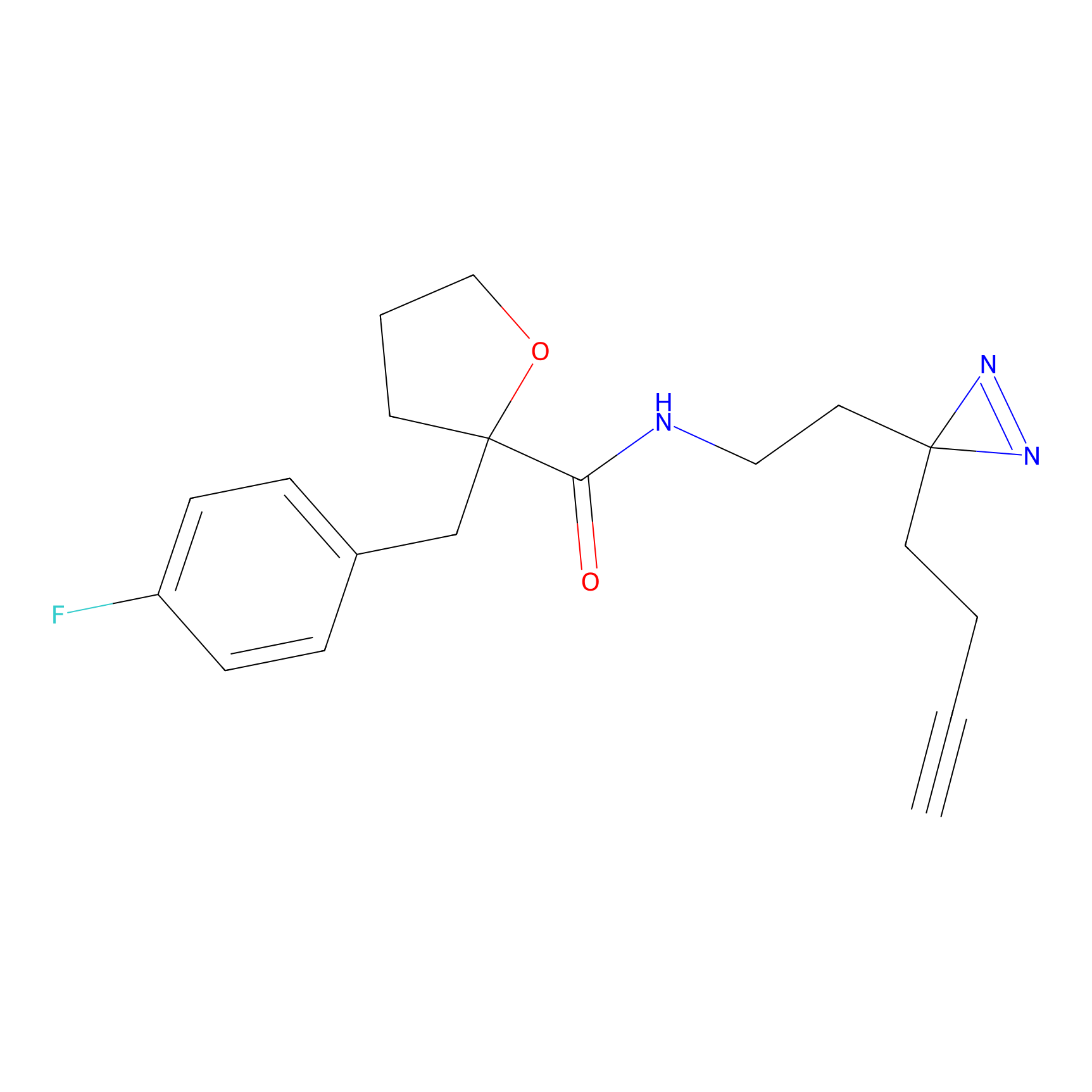
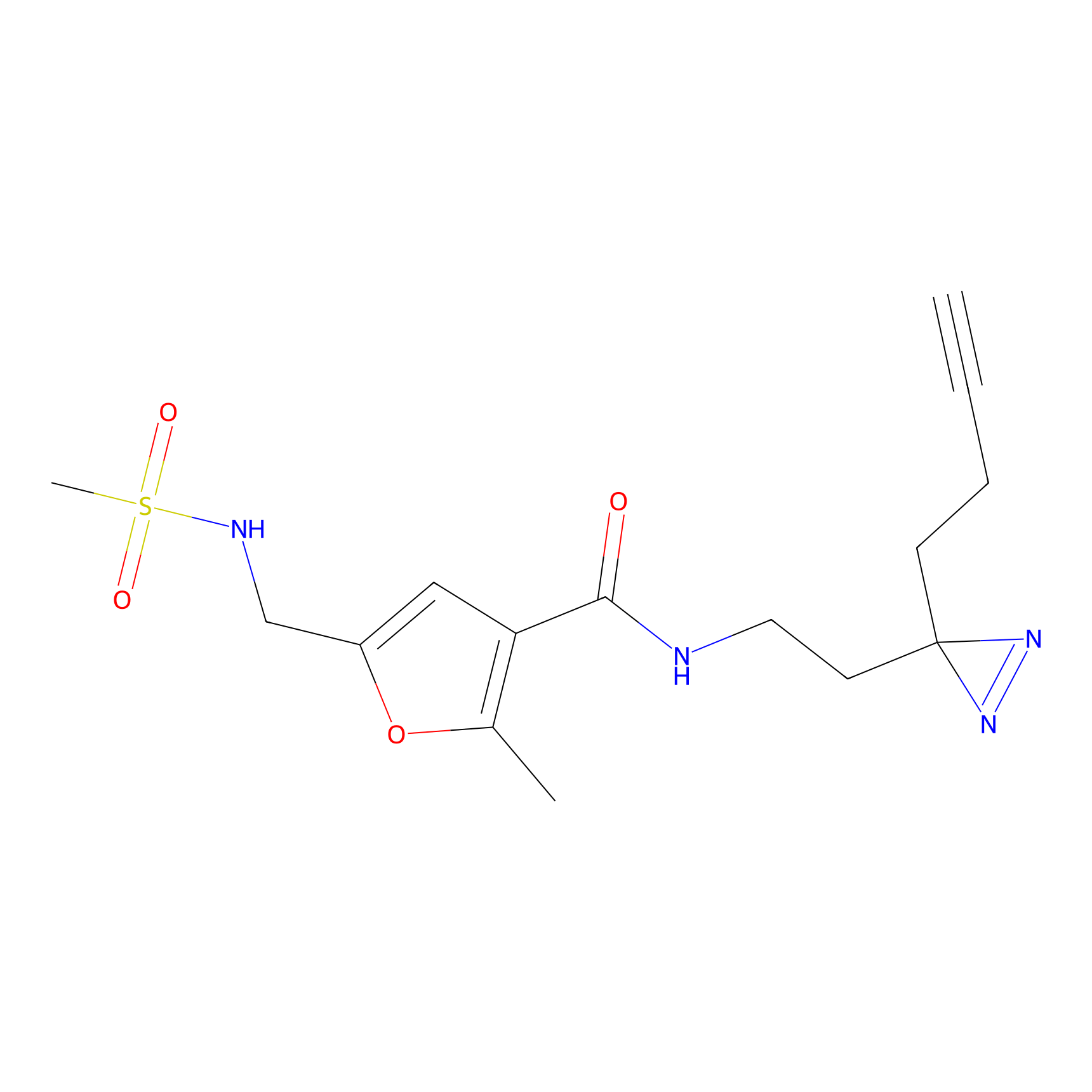
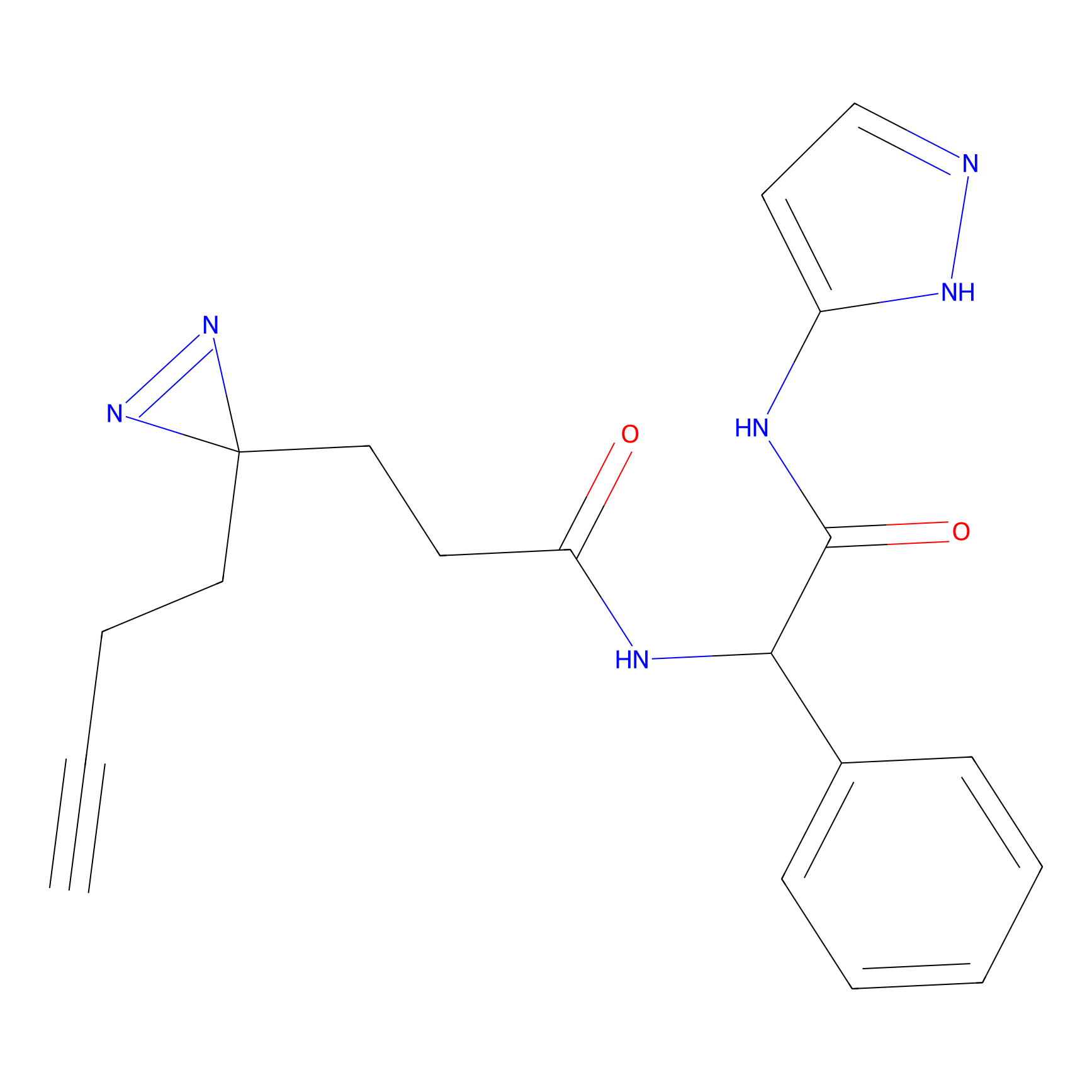
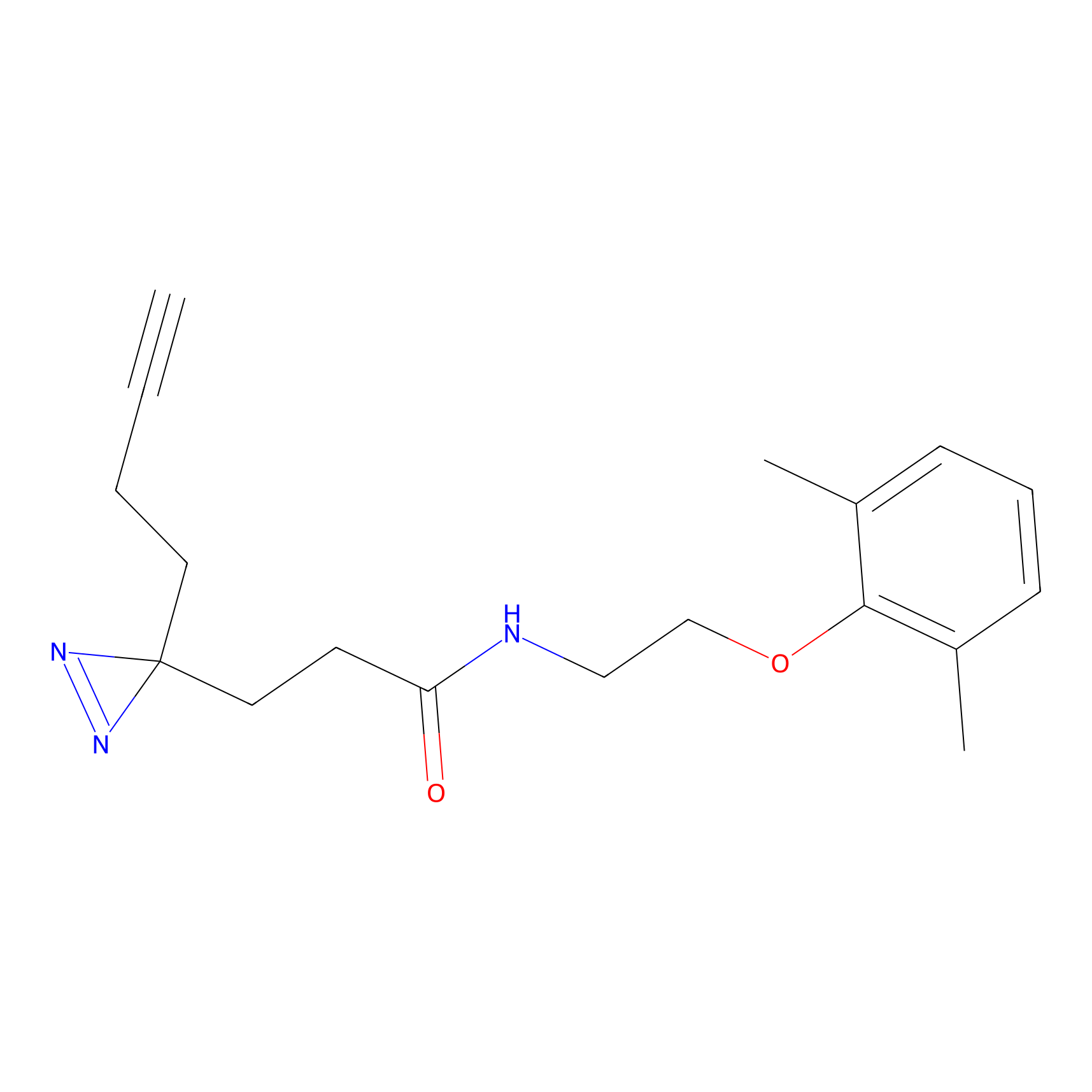
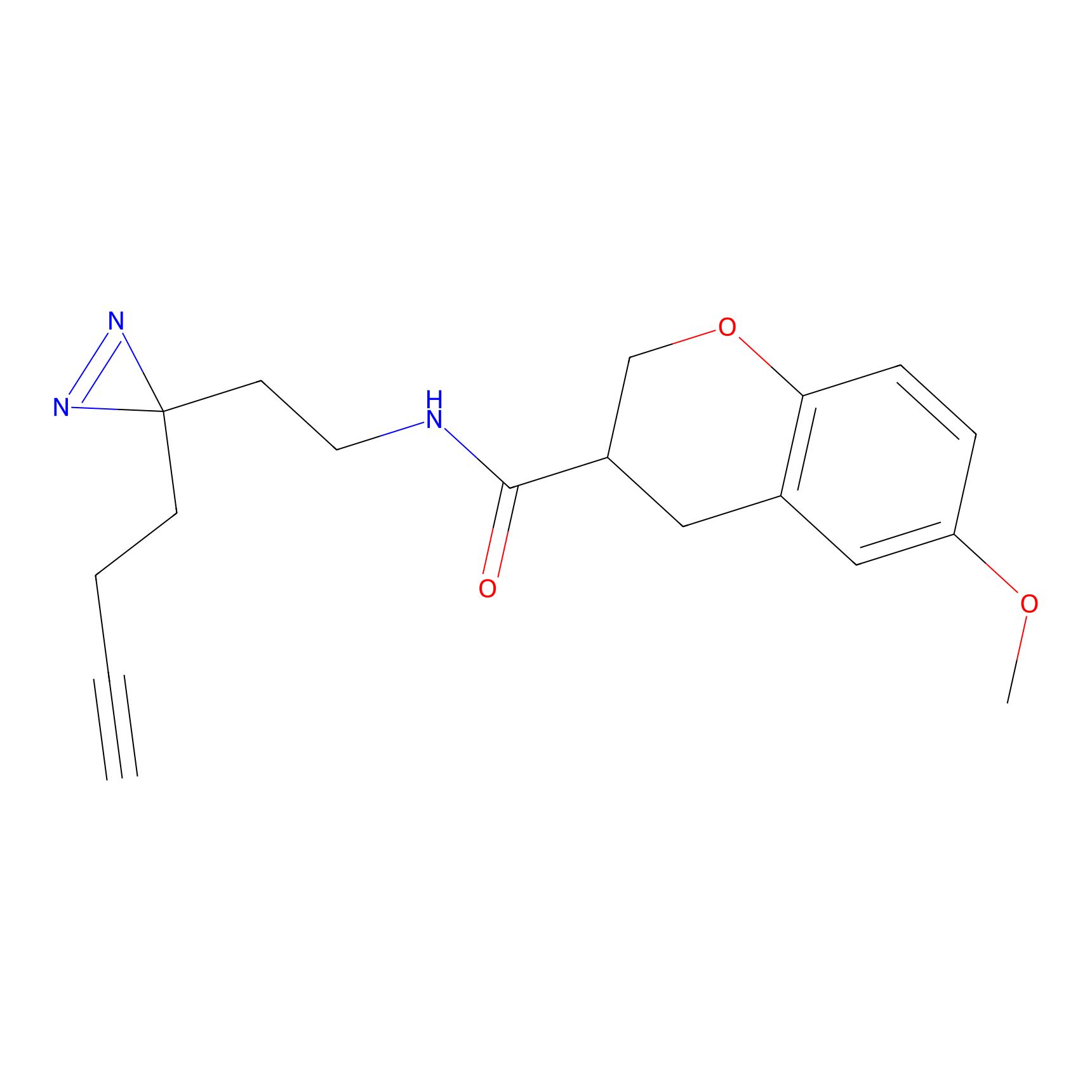
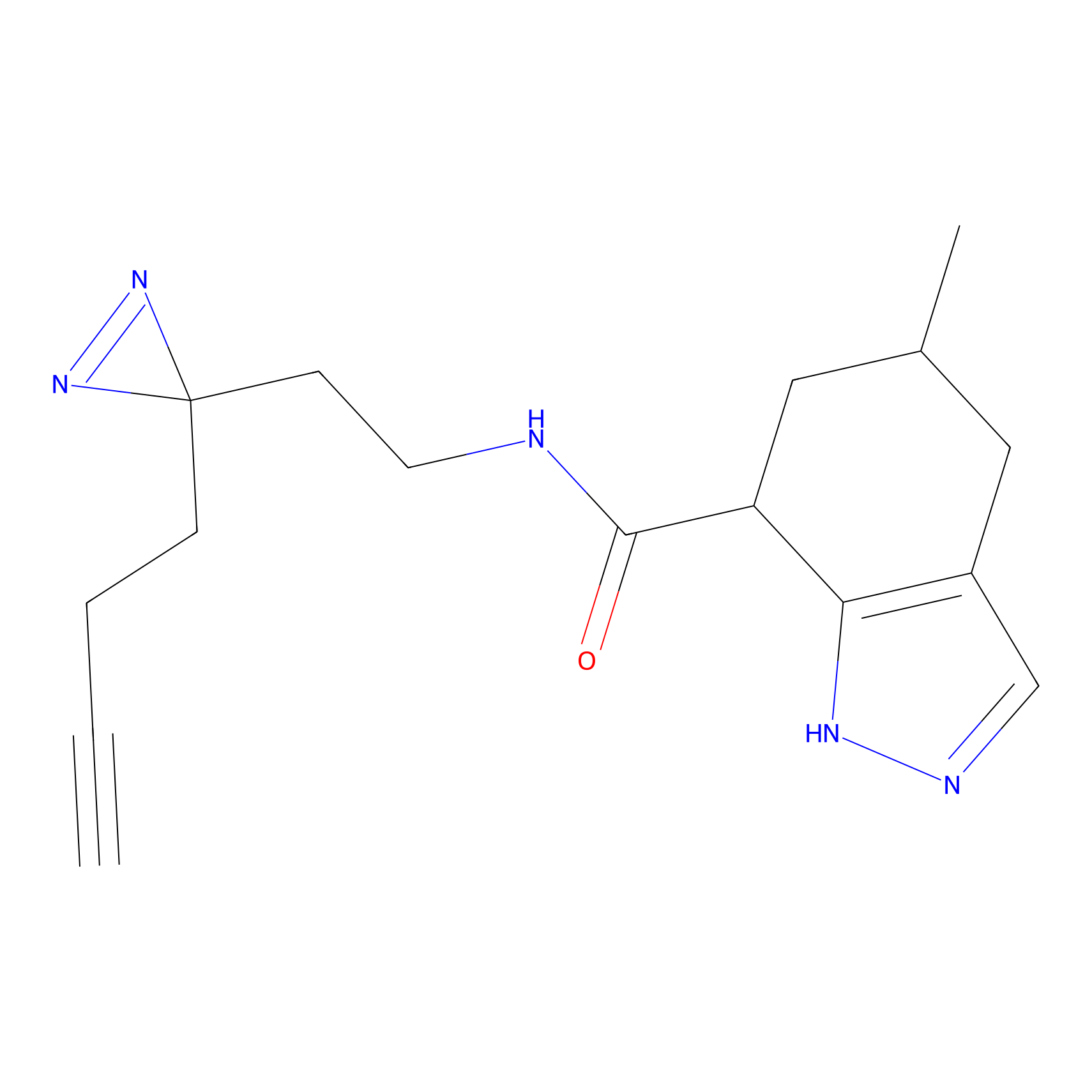
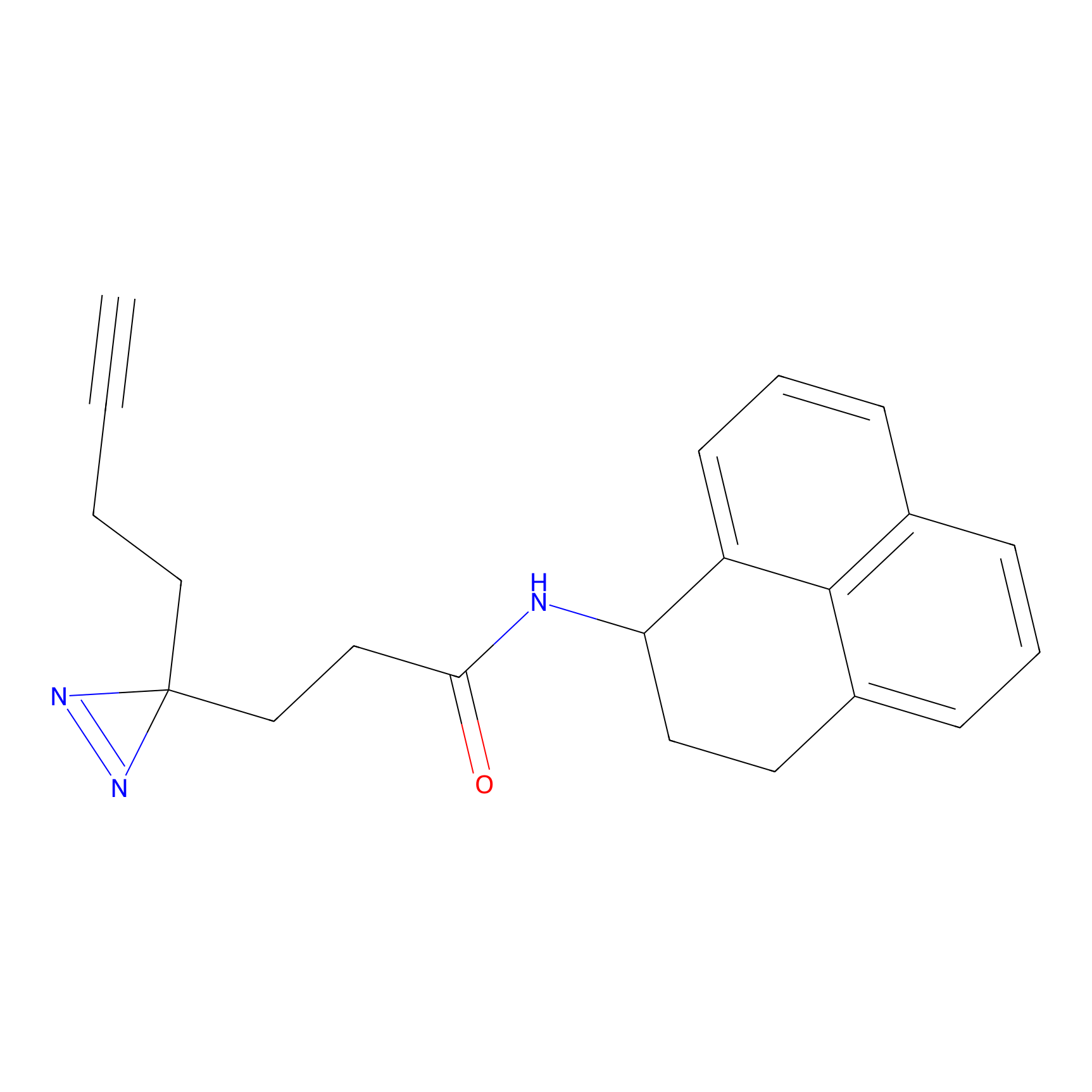
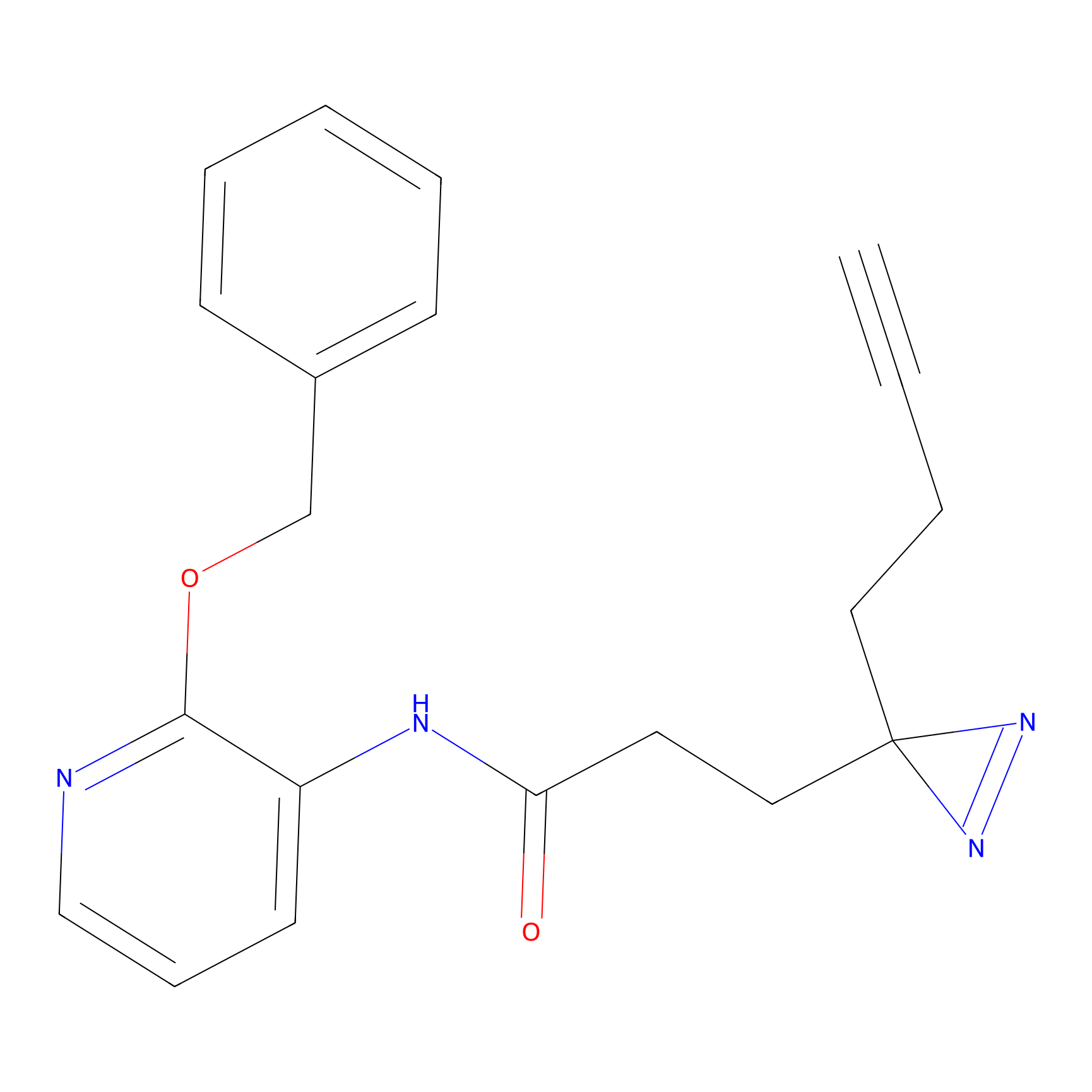
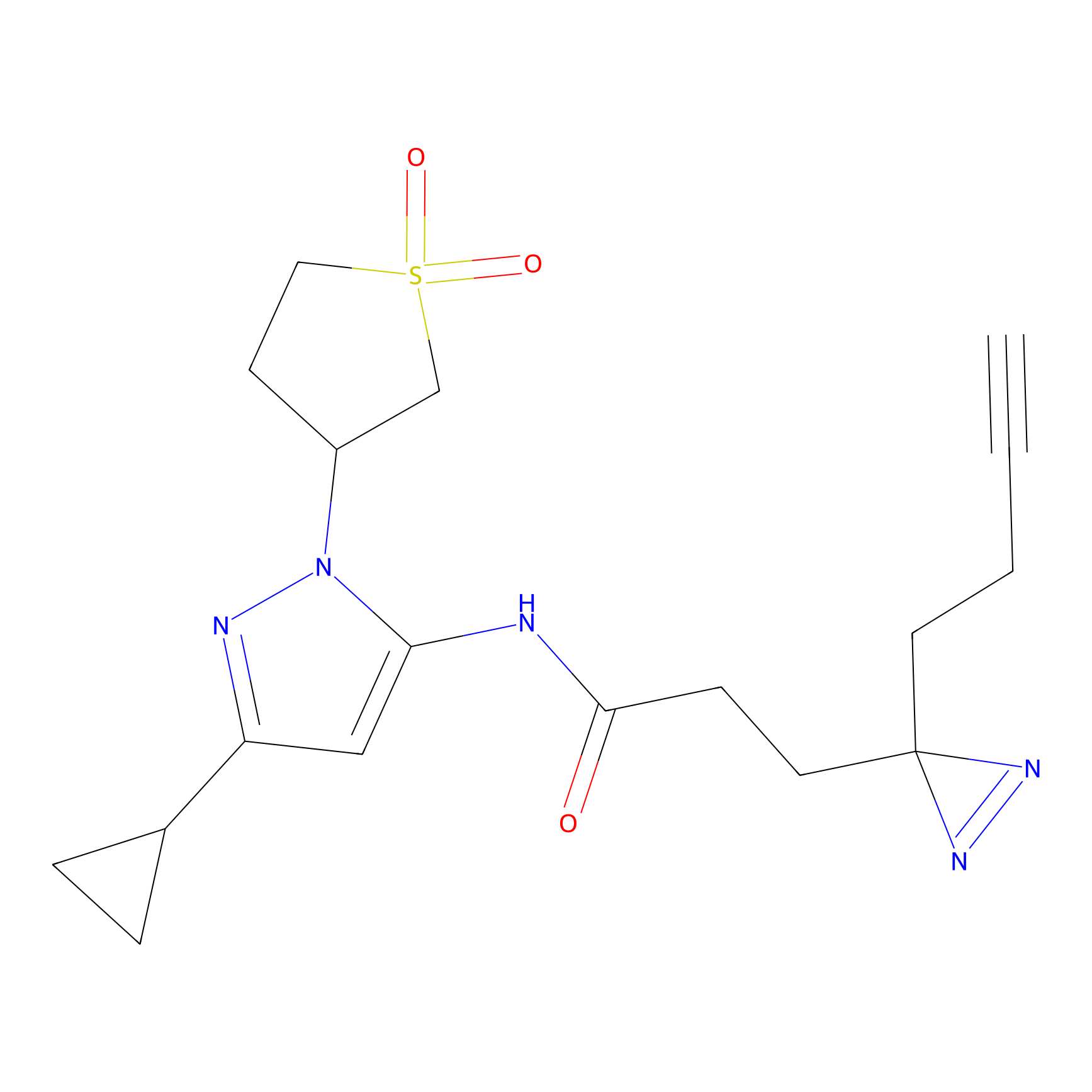
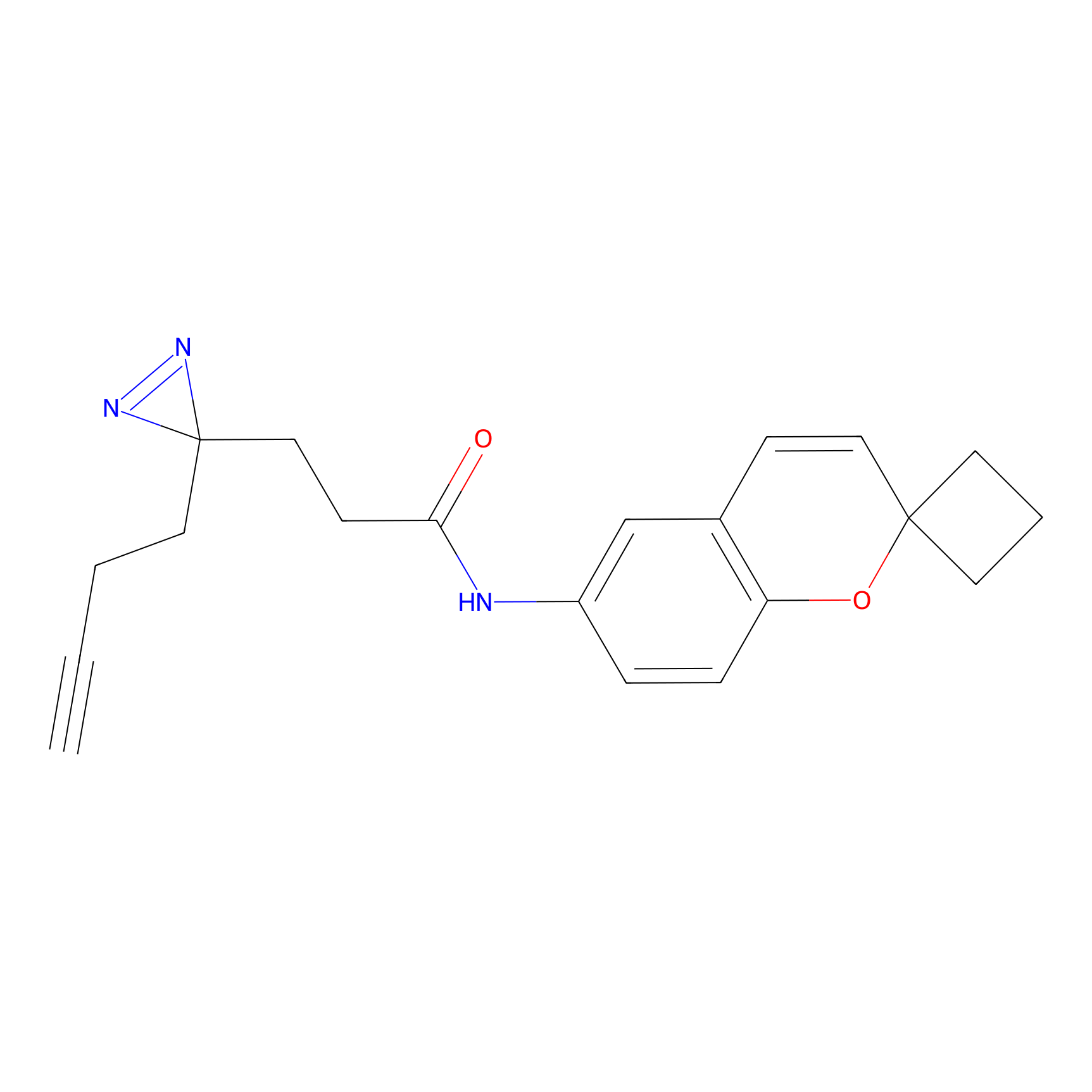
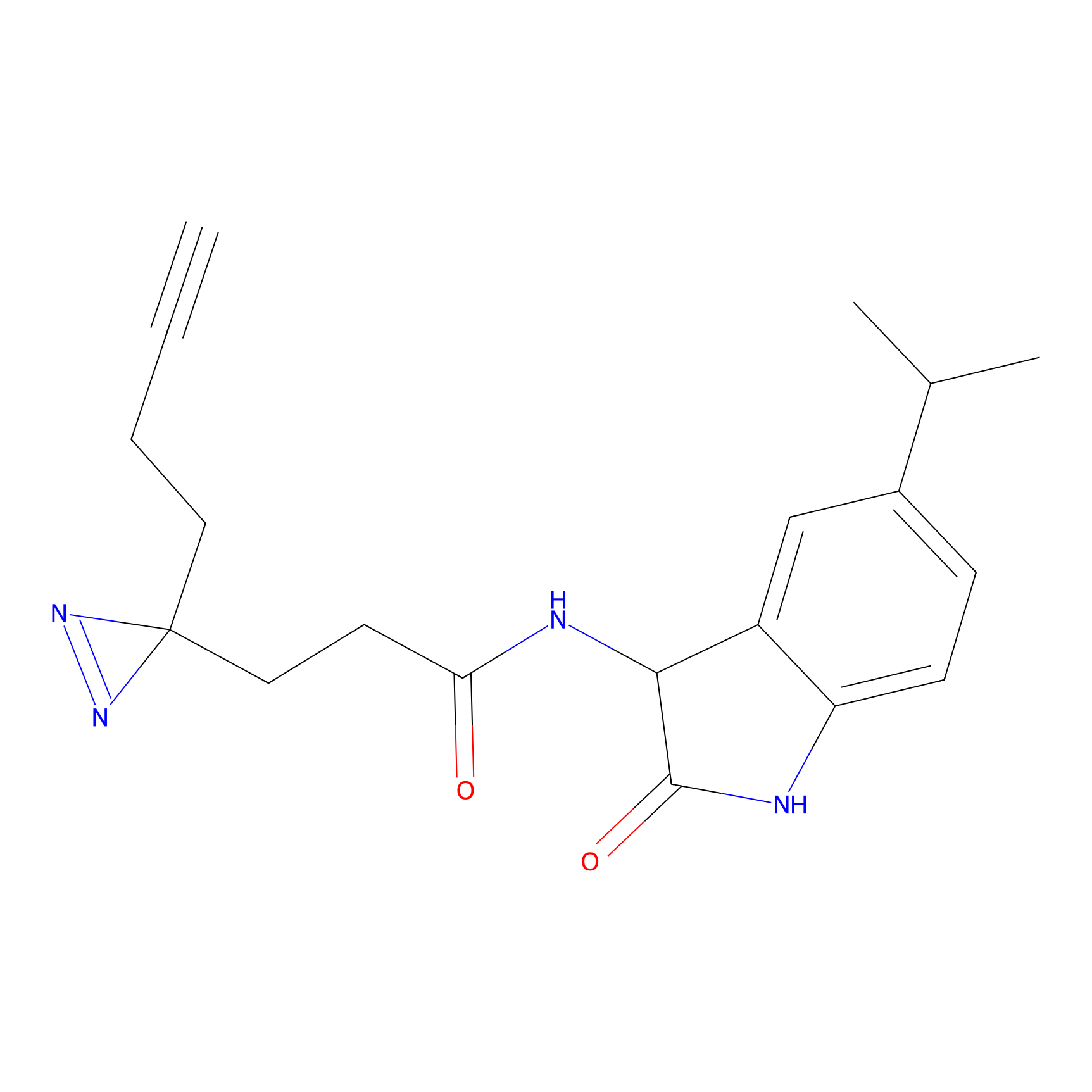
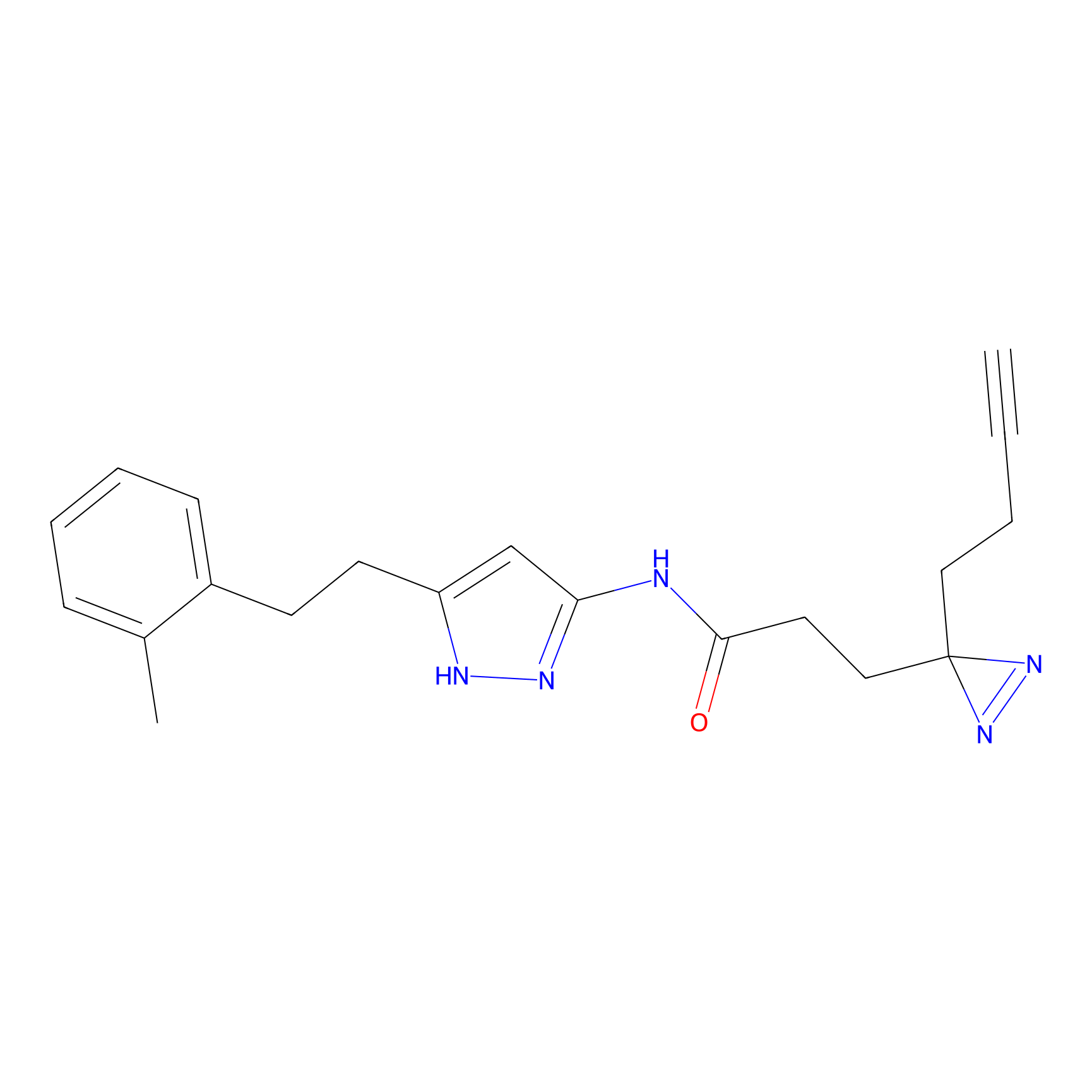
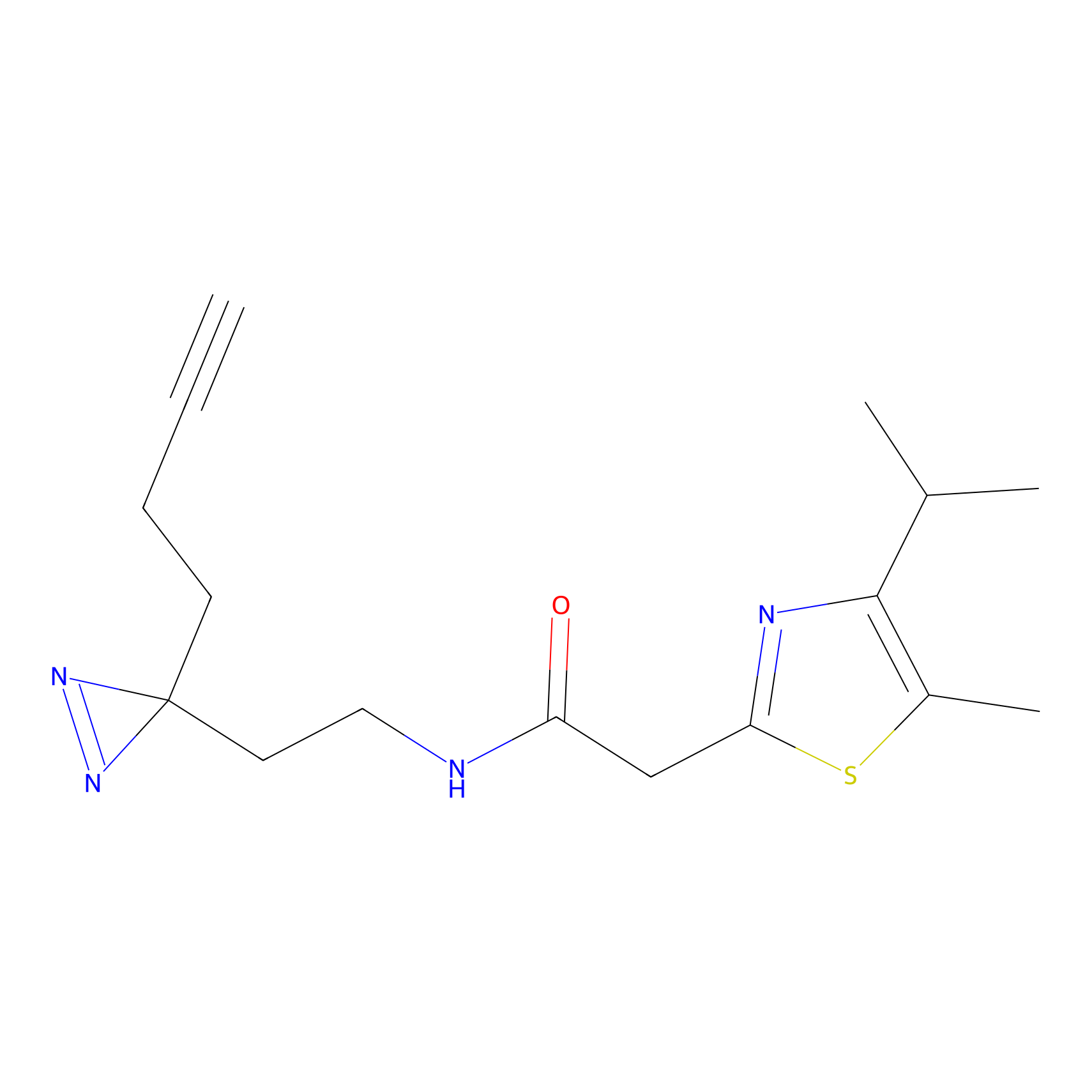
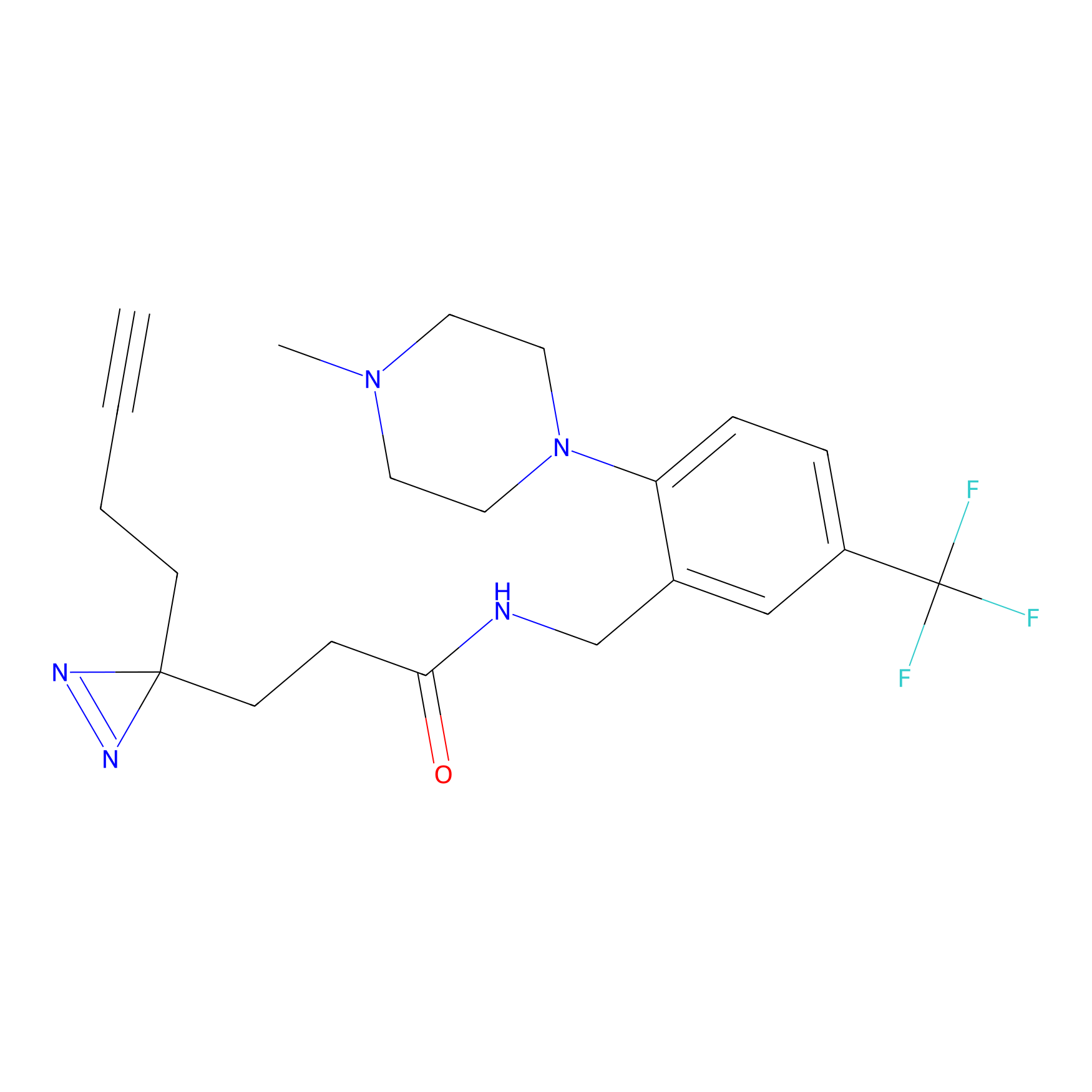
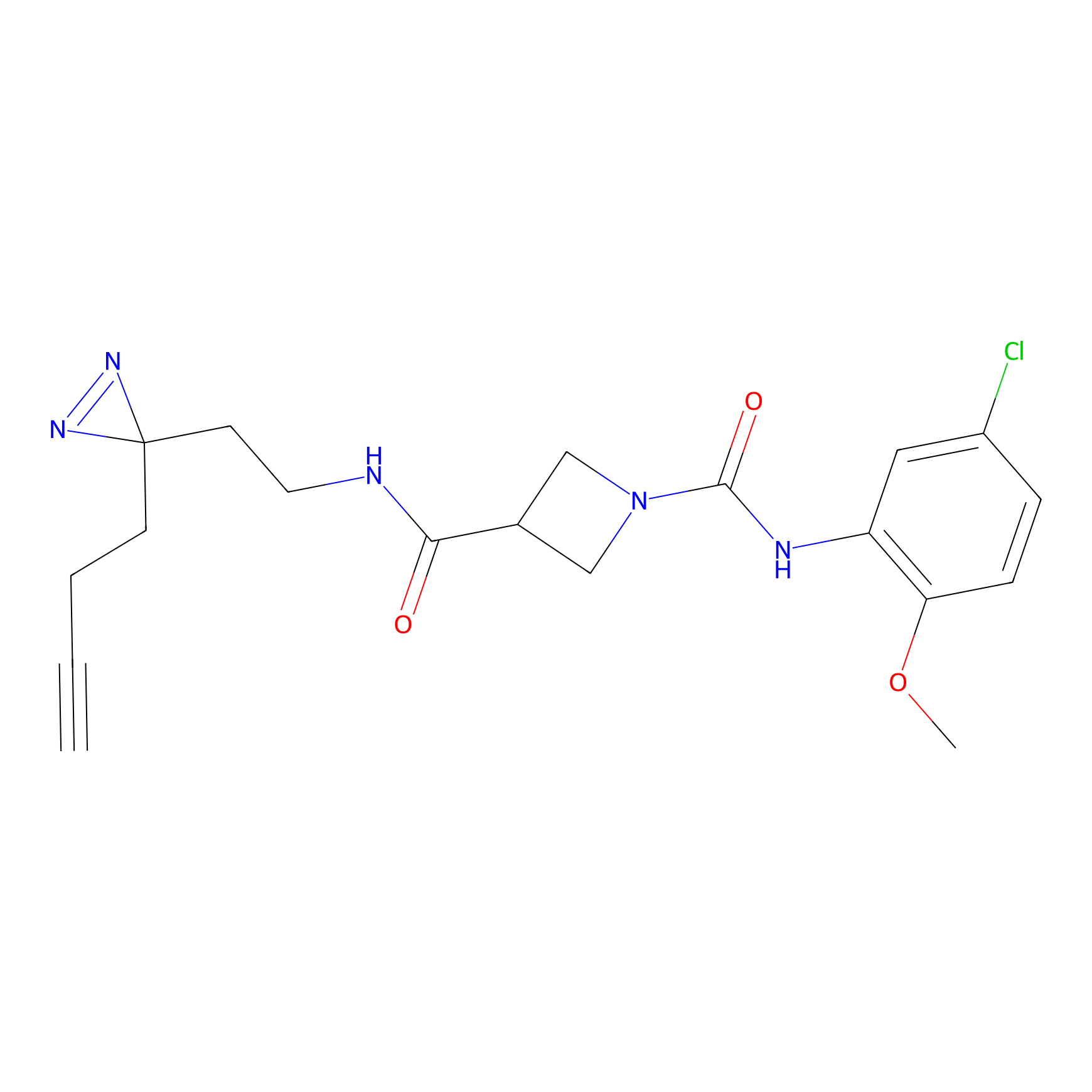
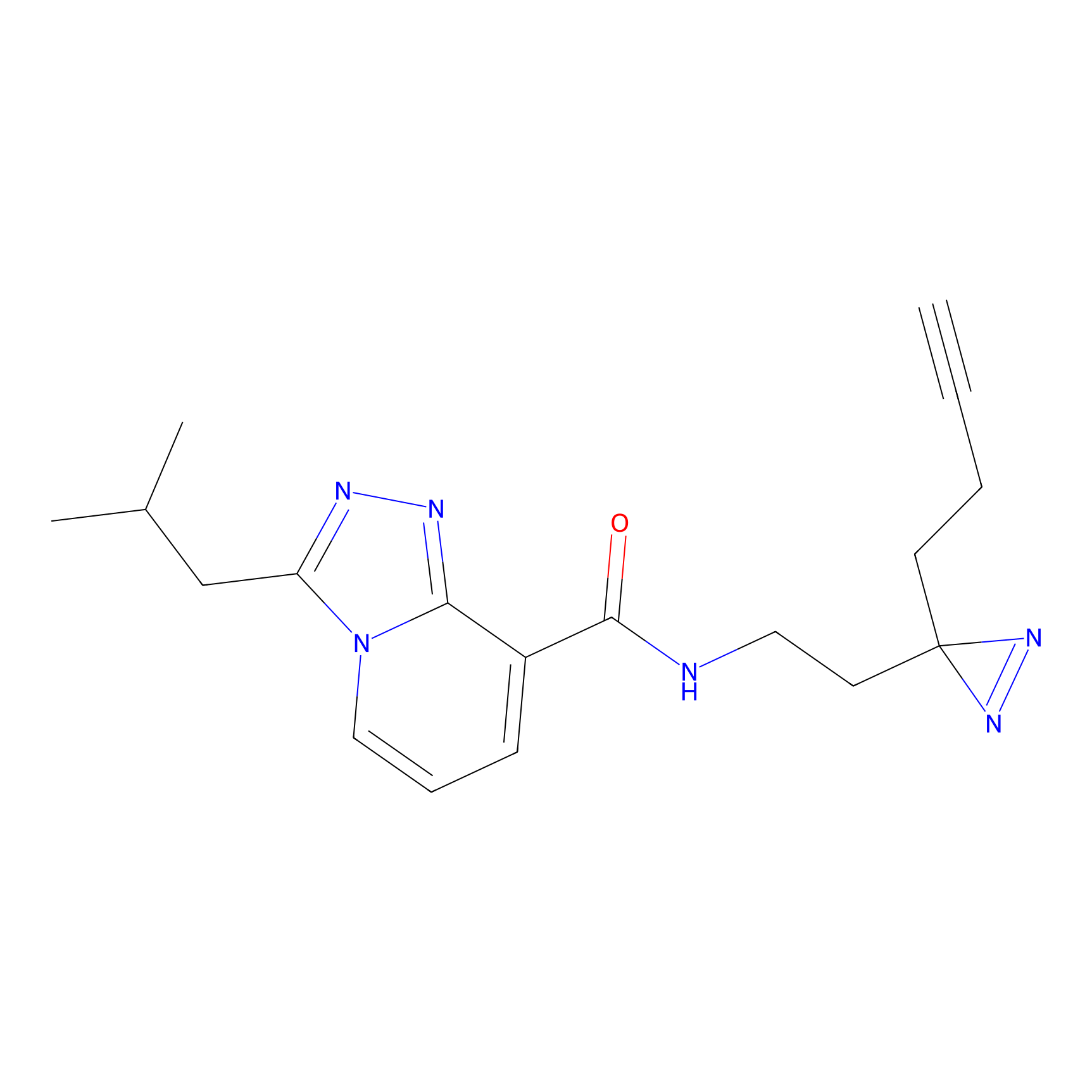
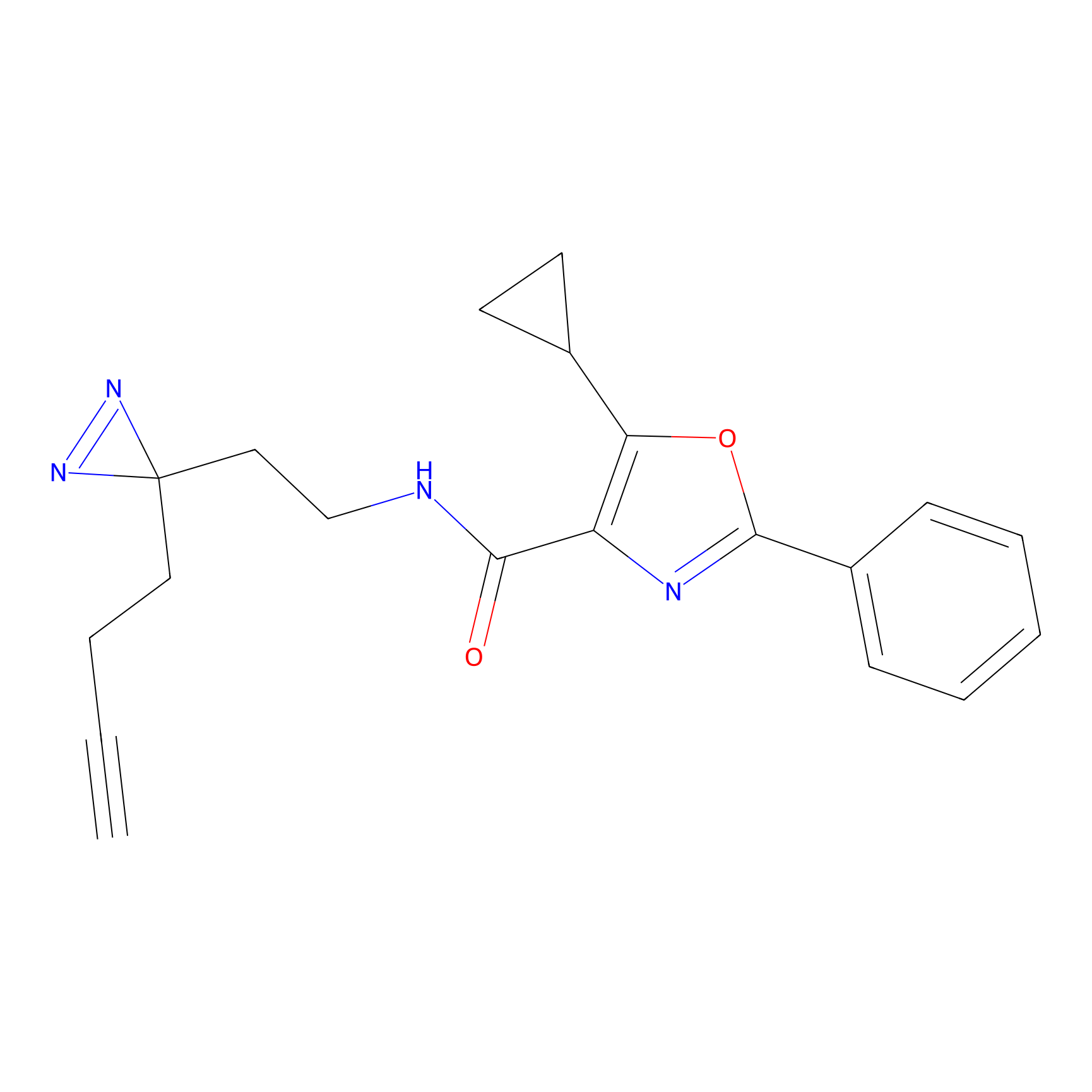
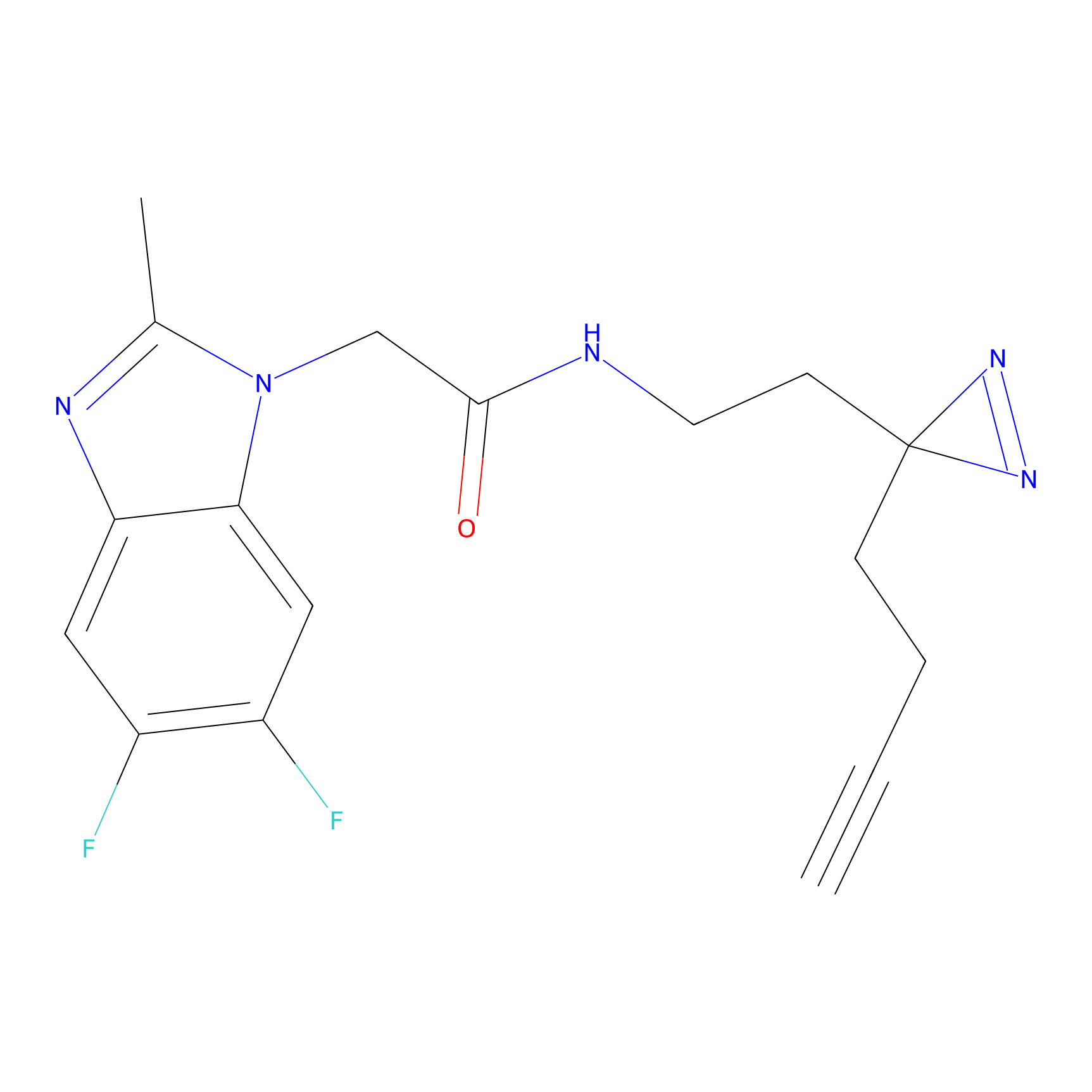
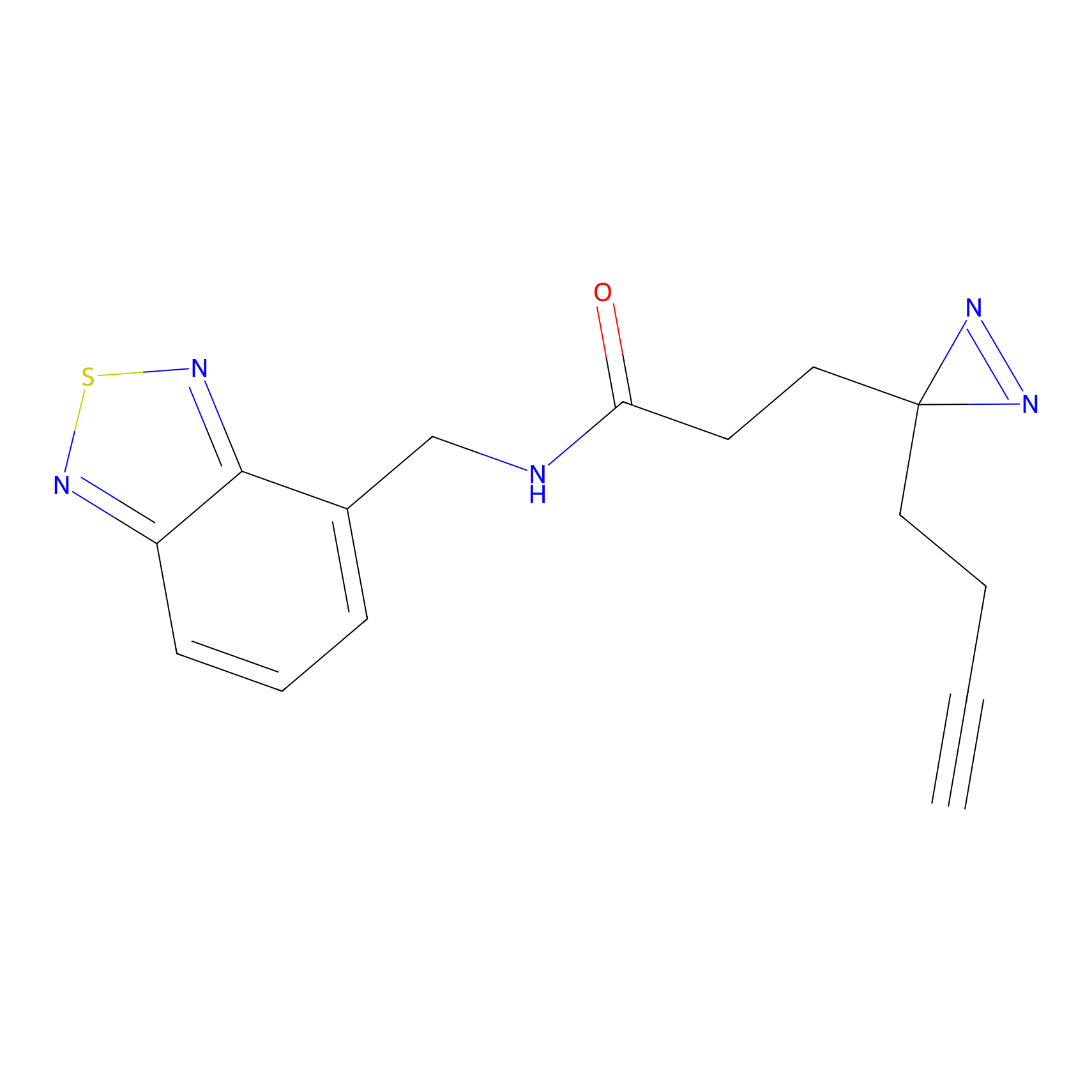
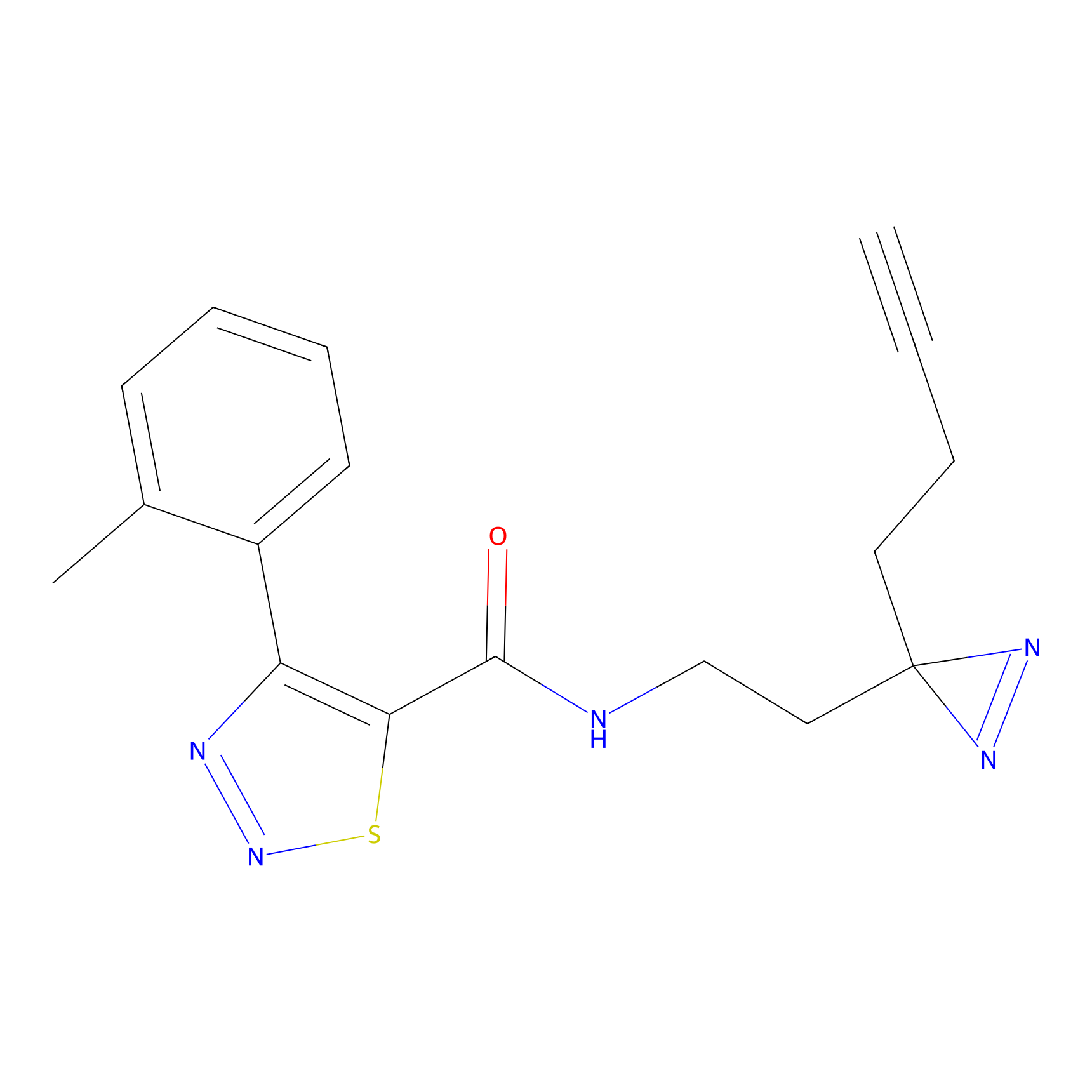
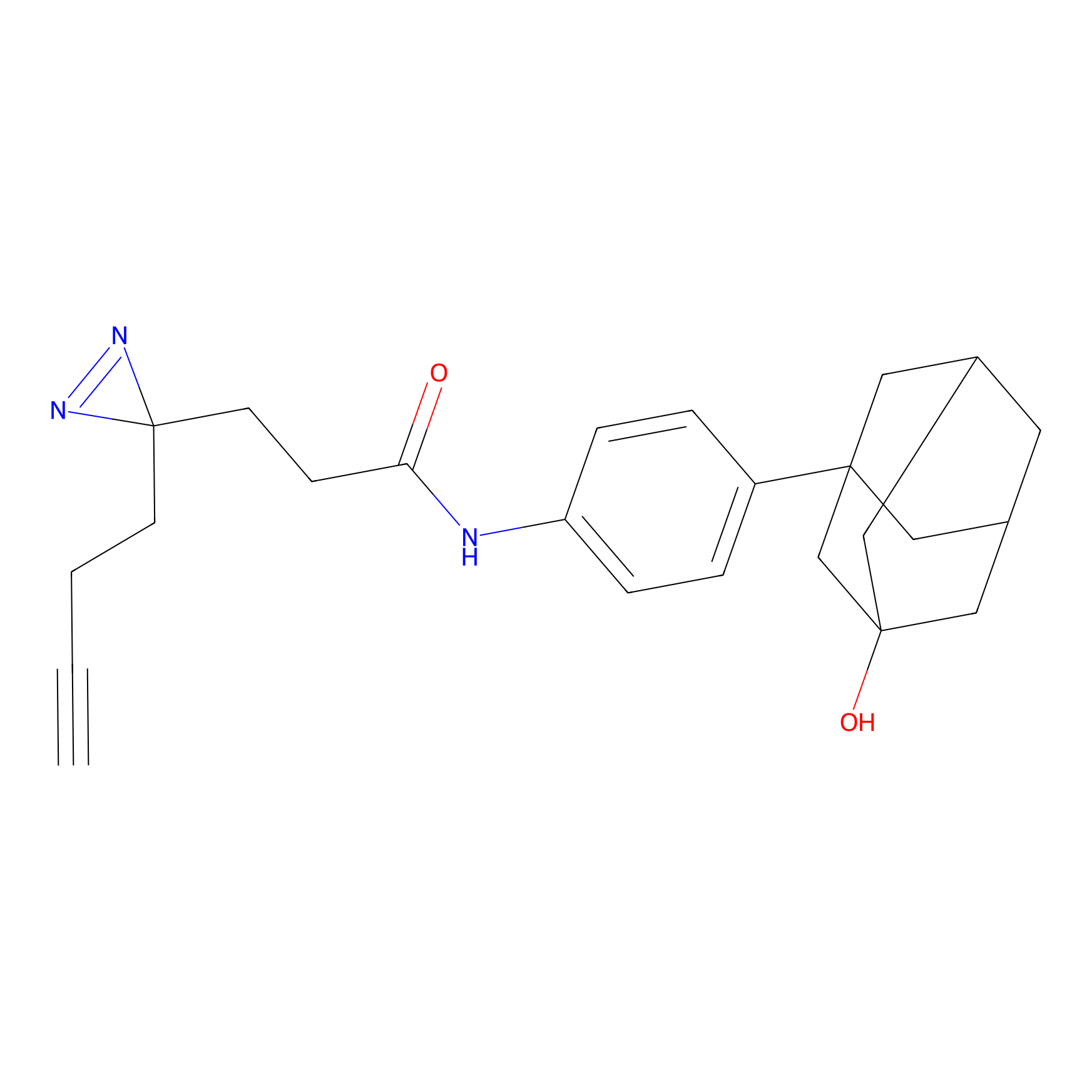
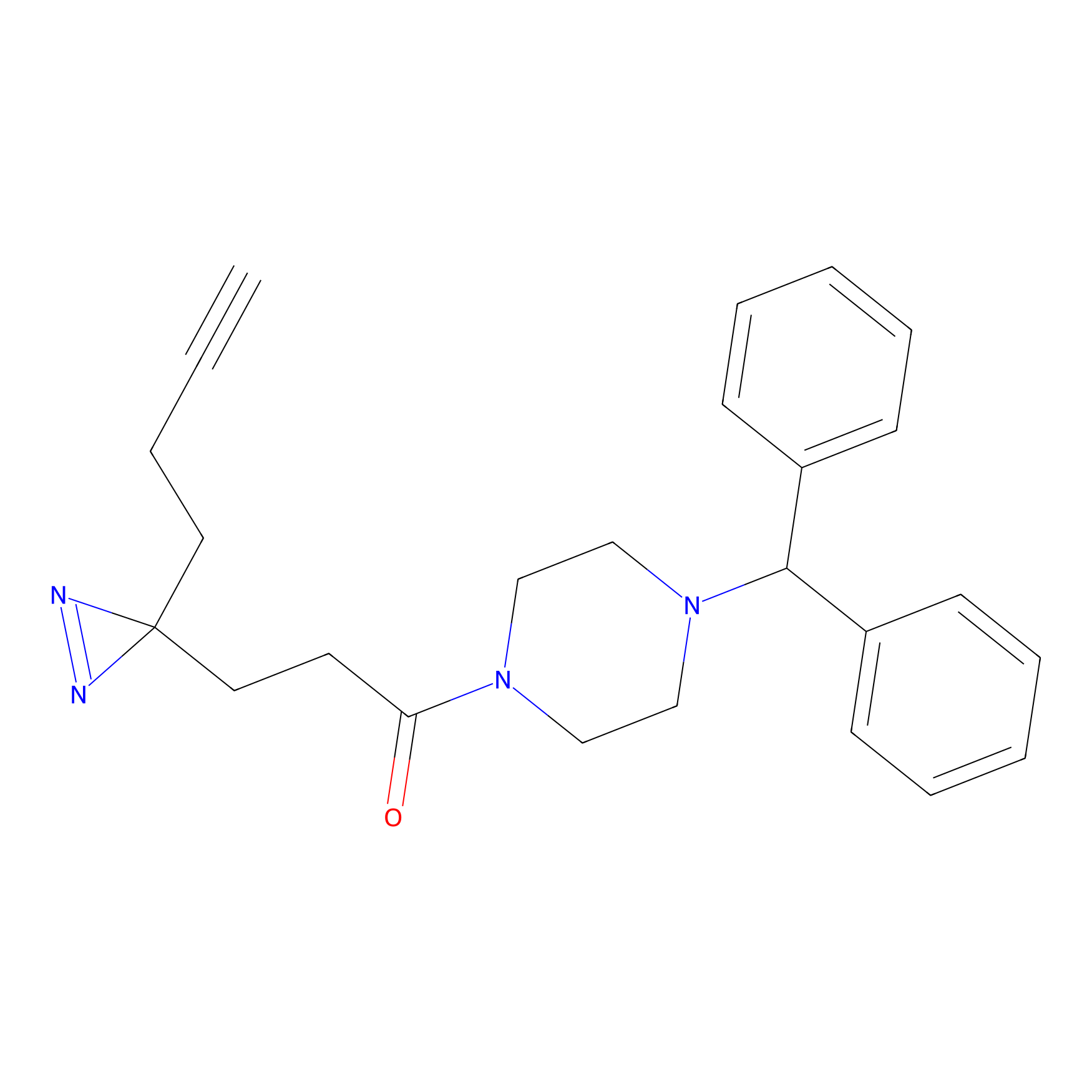
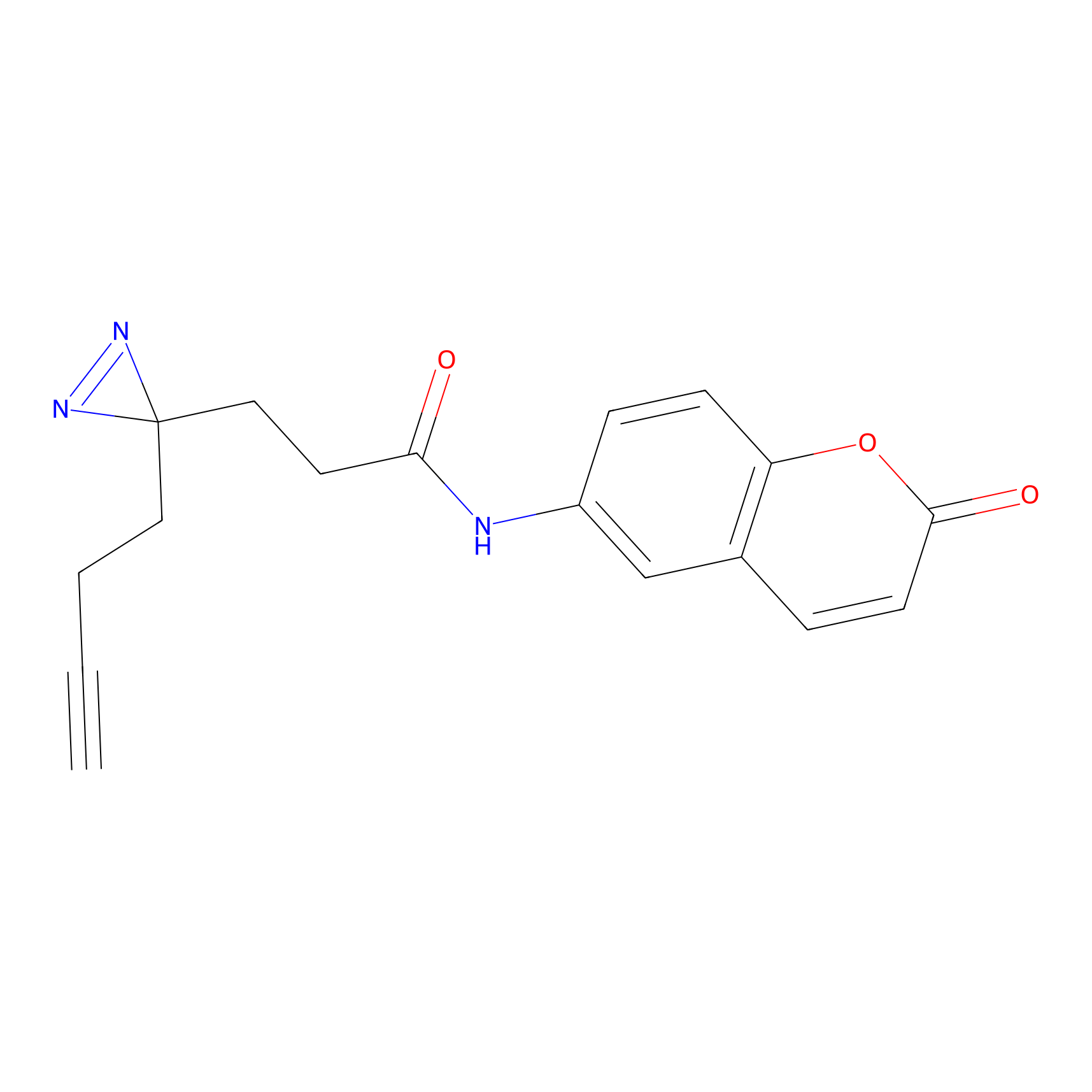
|
Crotonaldehyde Probe Info |
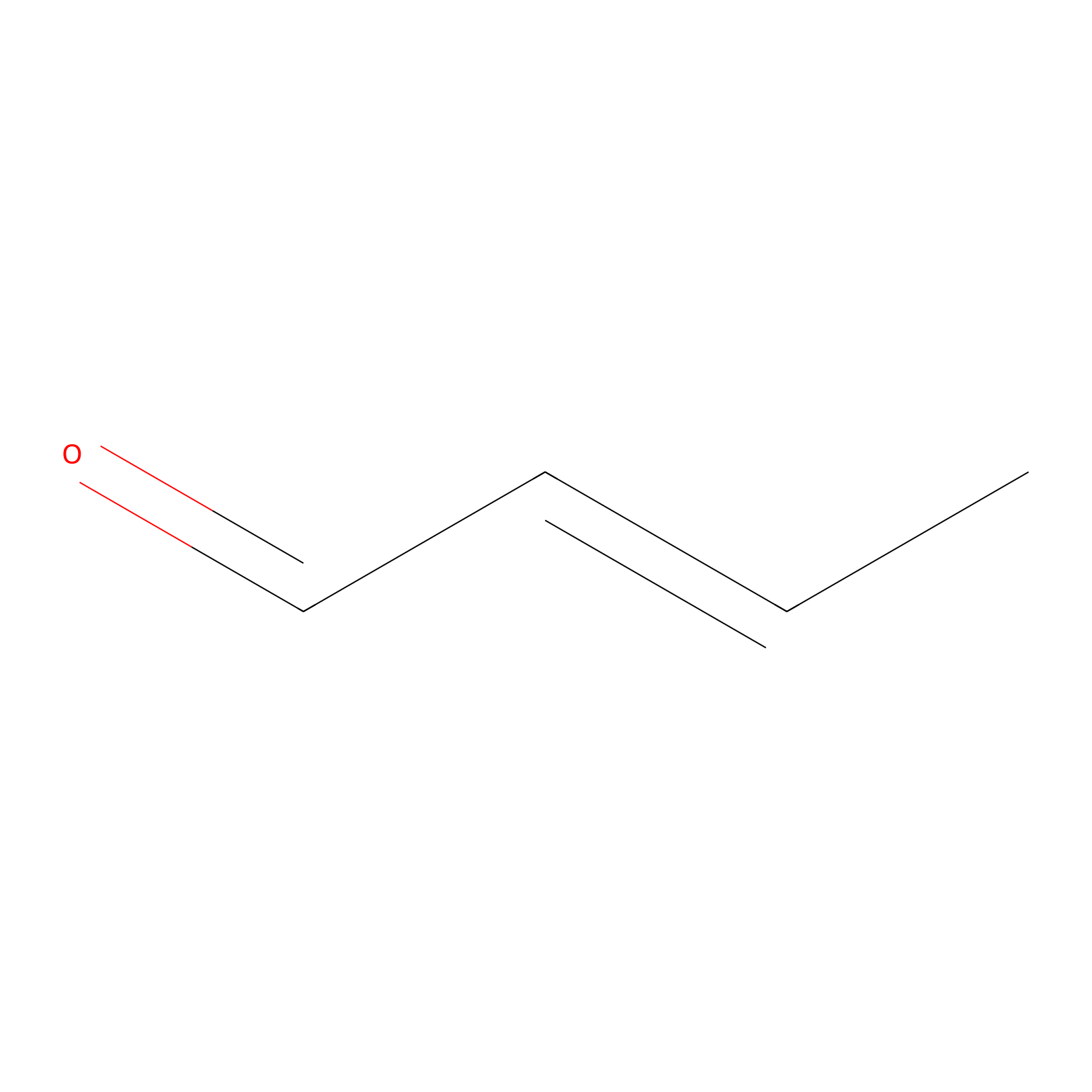 |
N.A. | LDD0219 | [2] | |
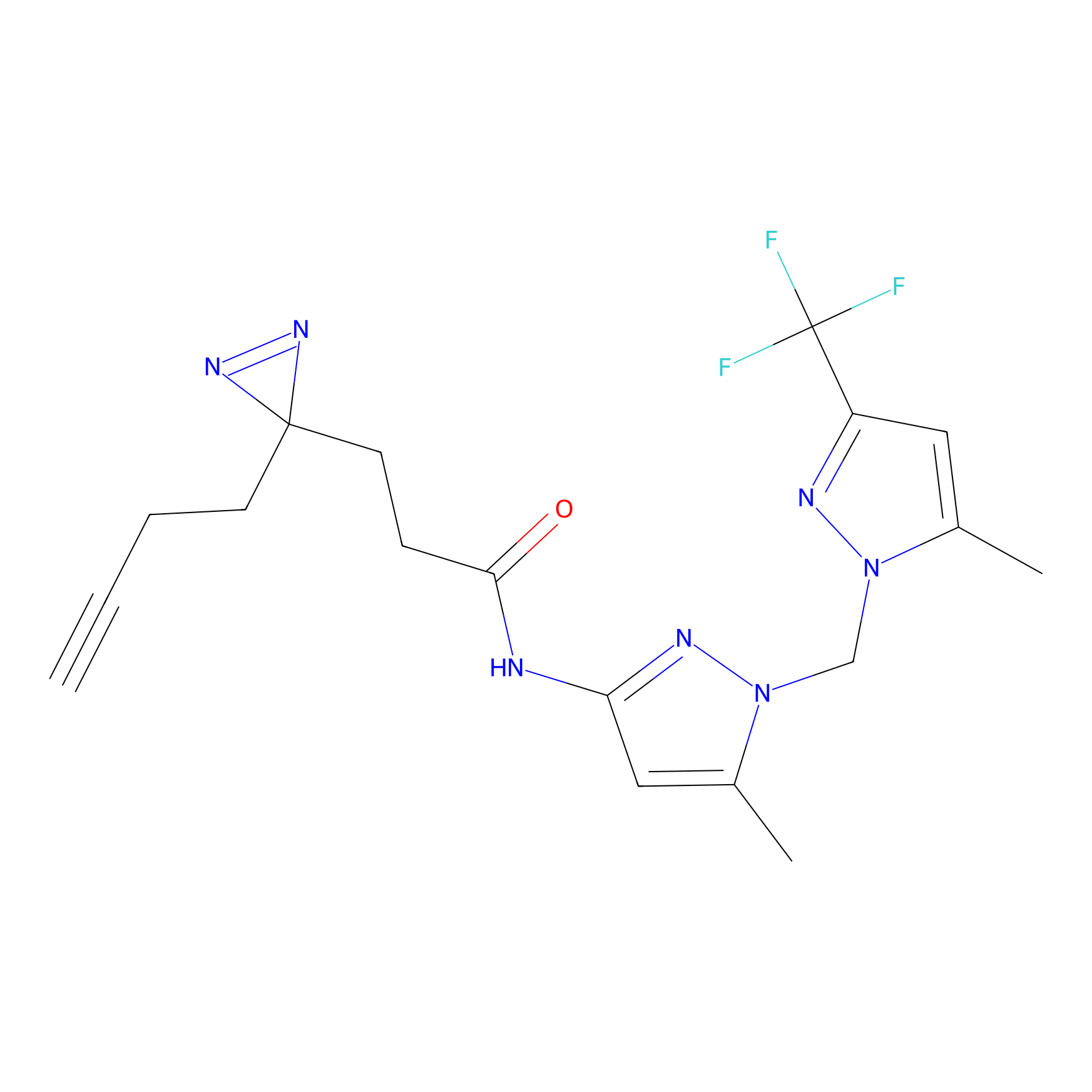
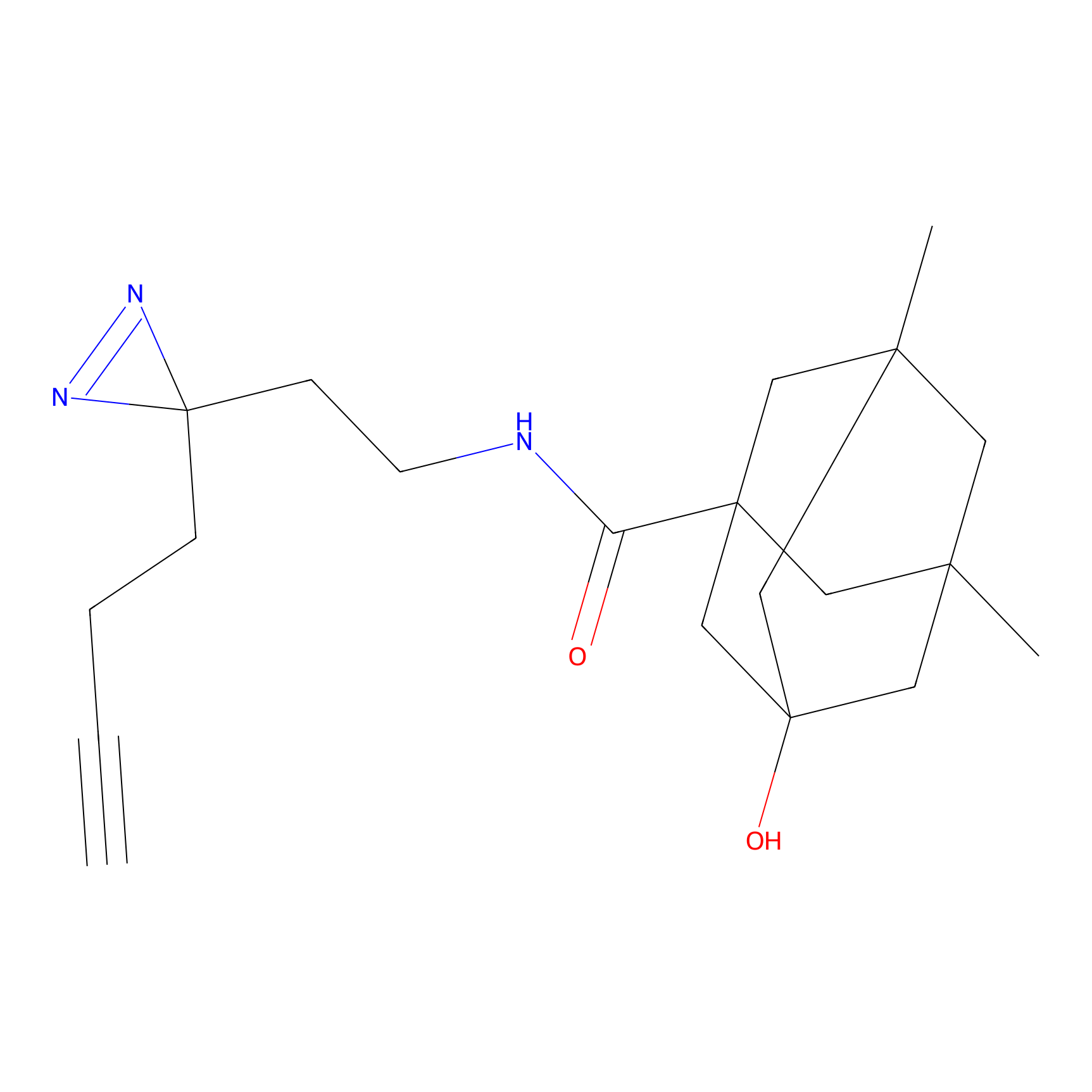
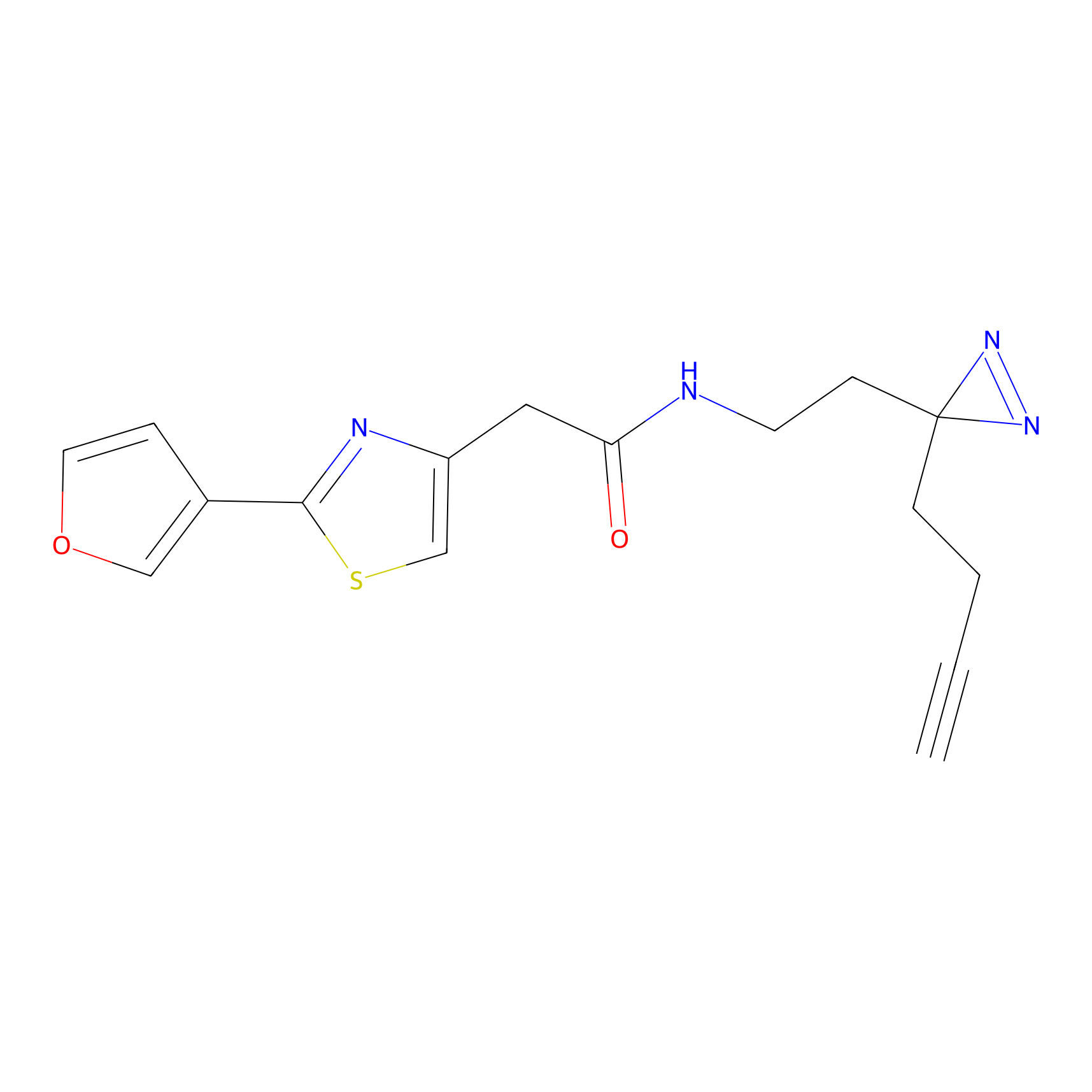
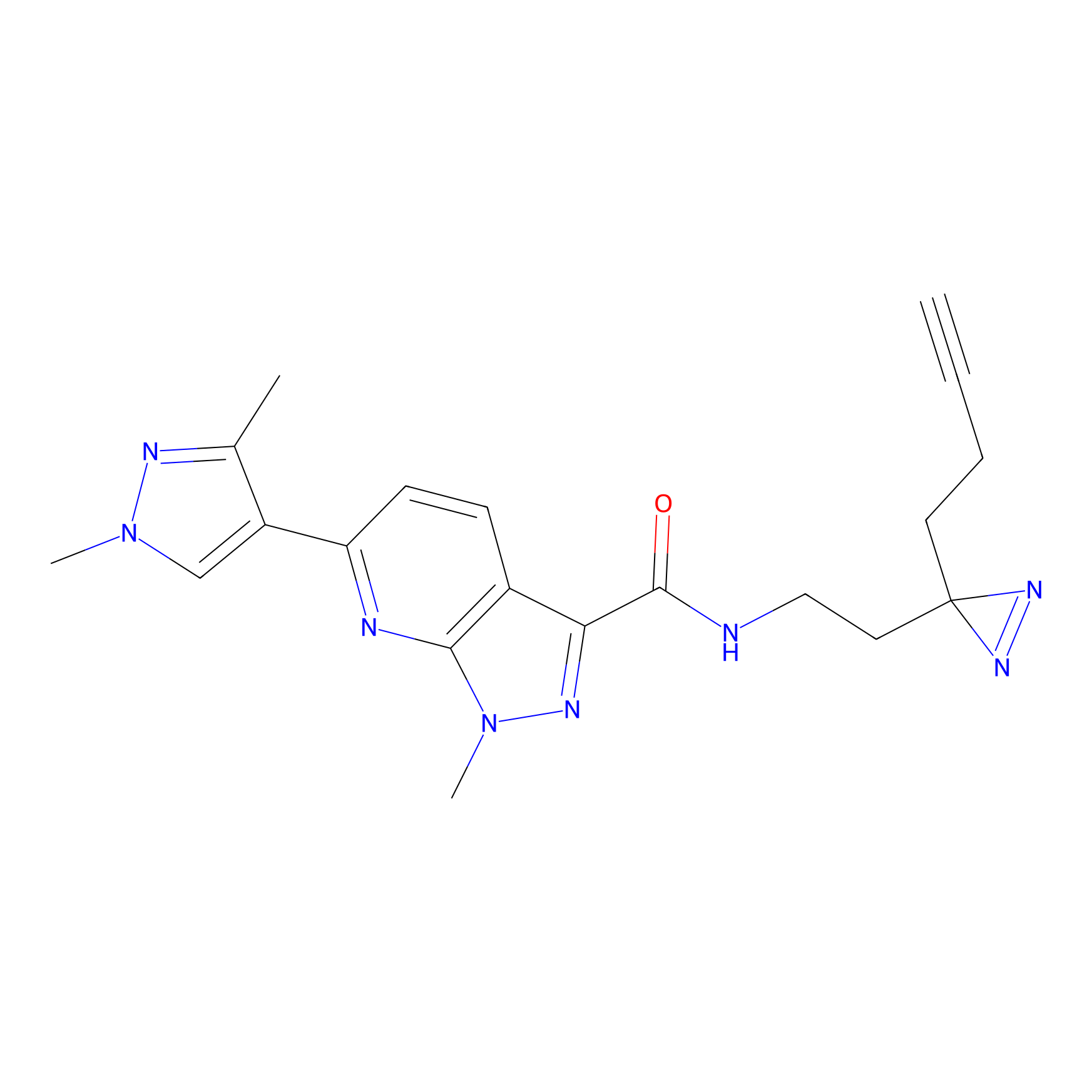
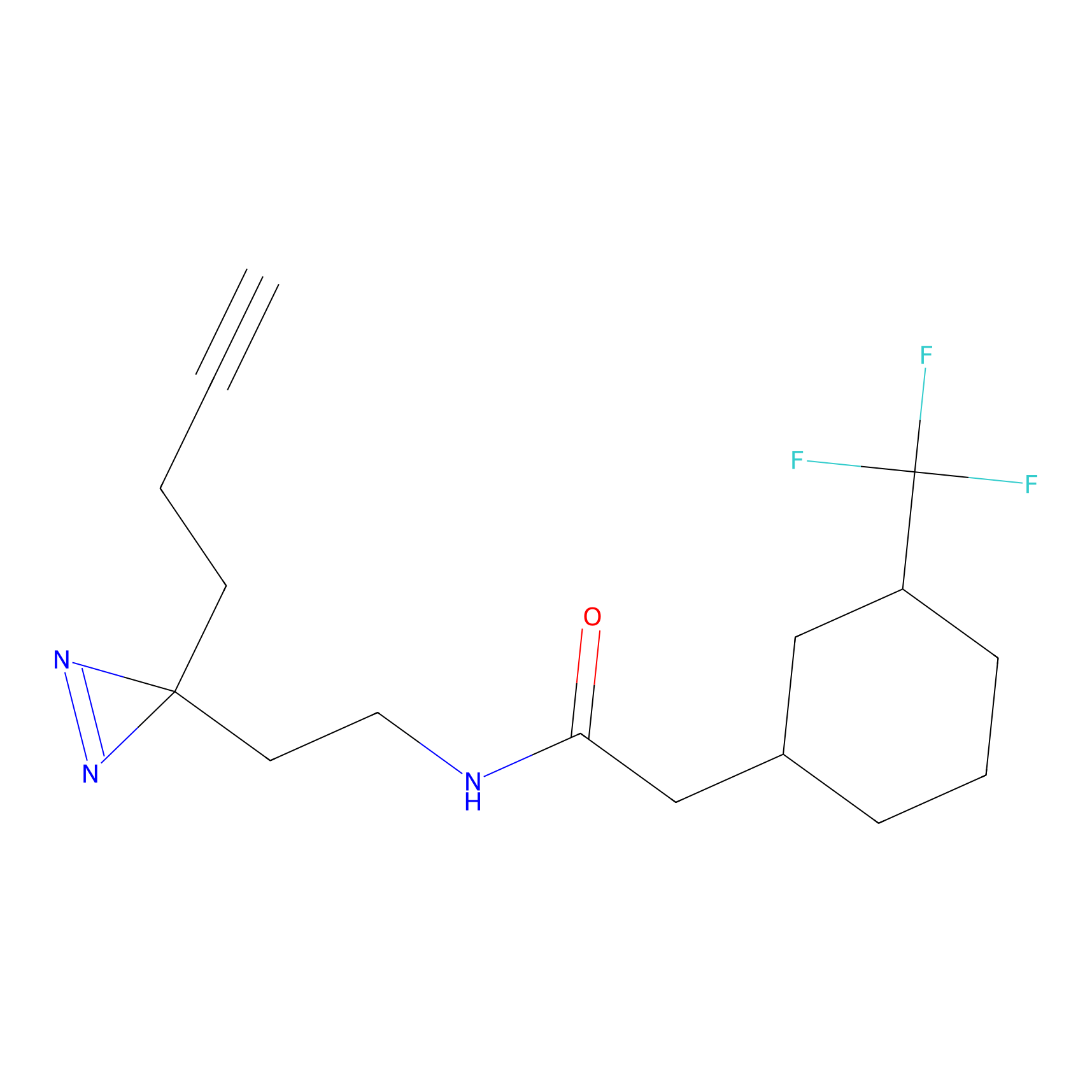
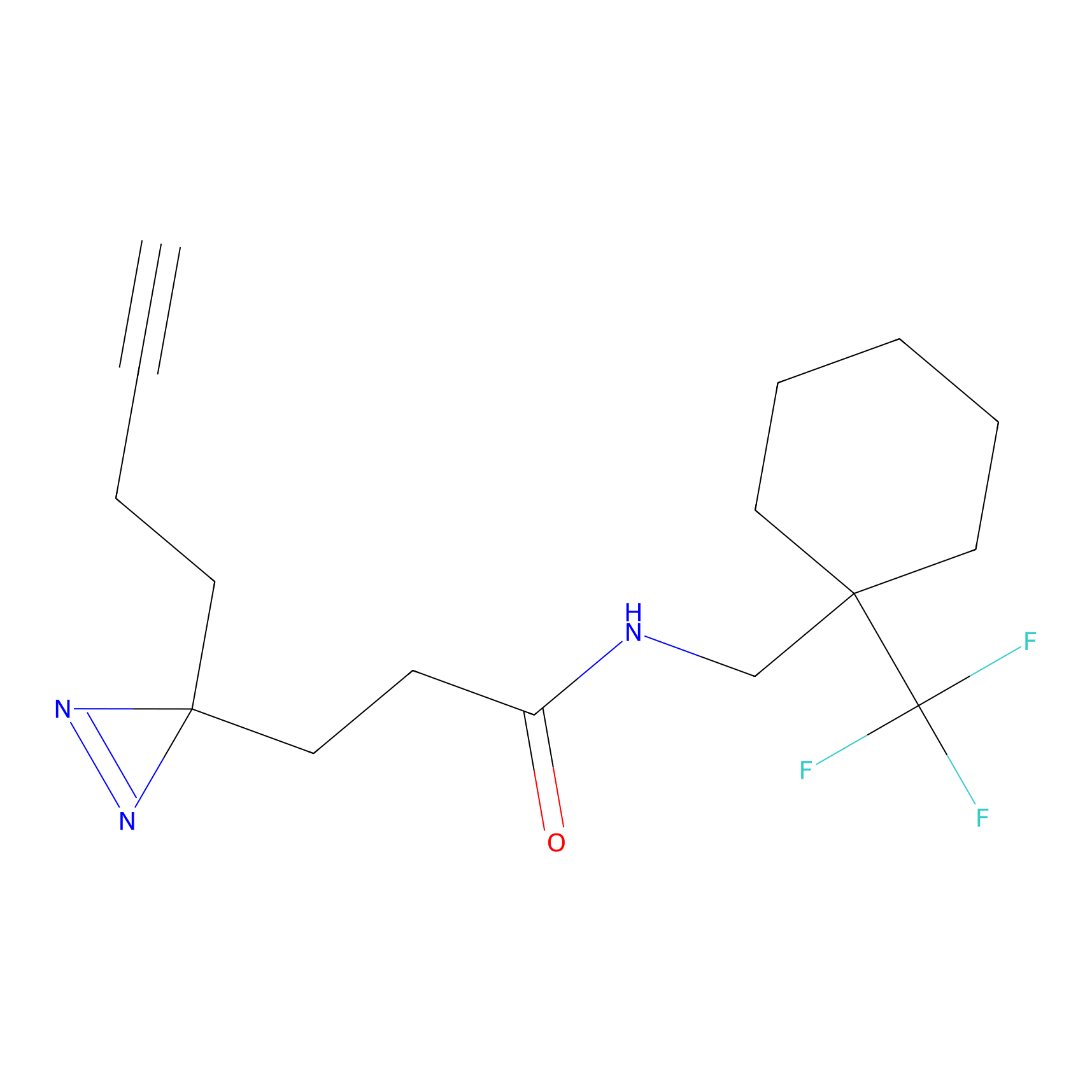
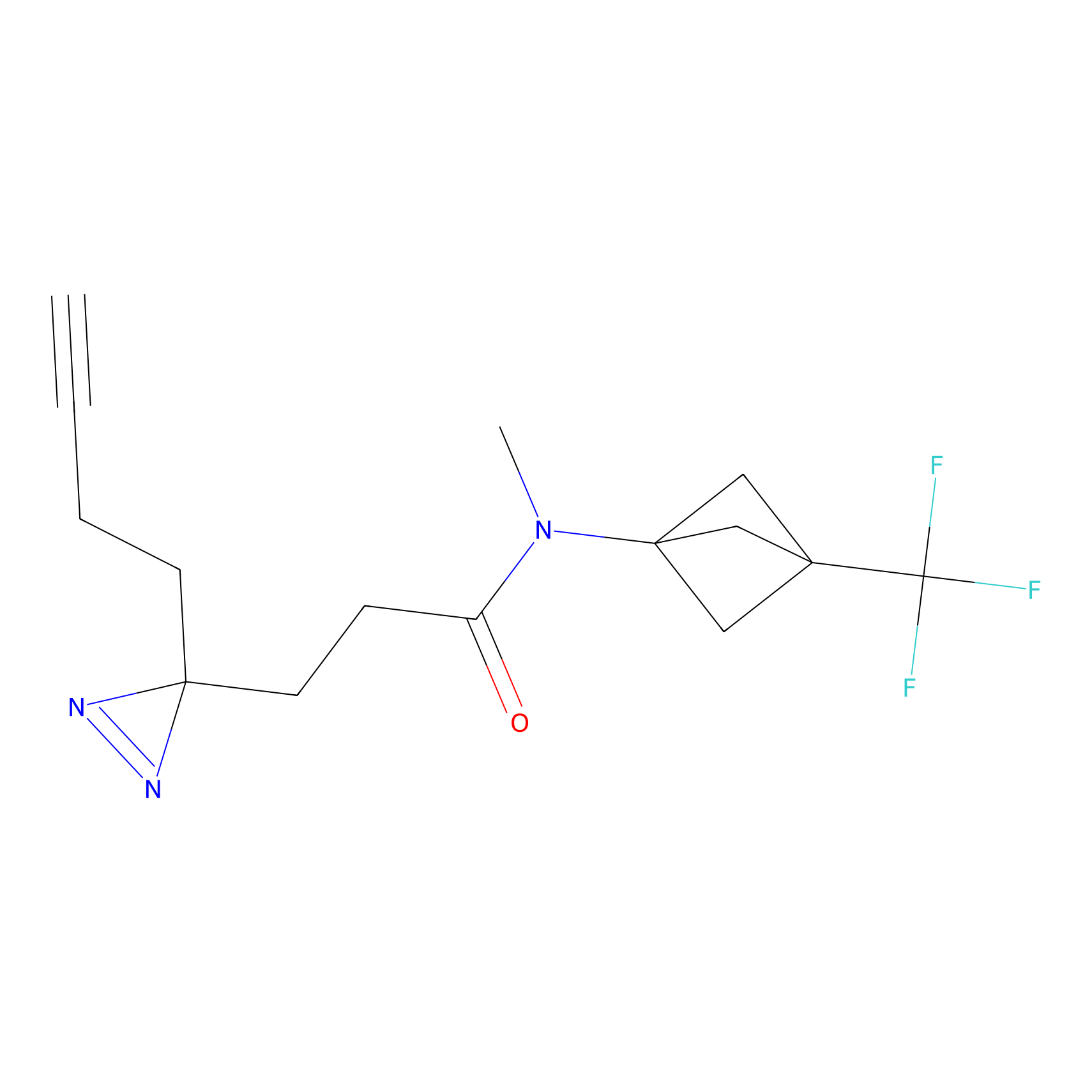
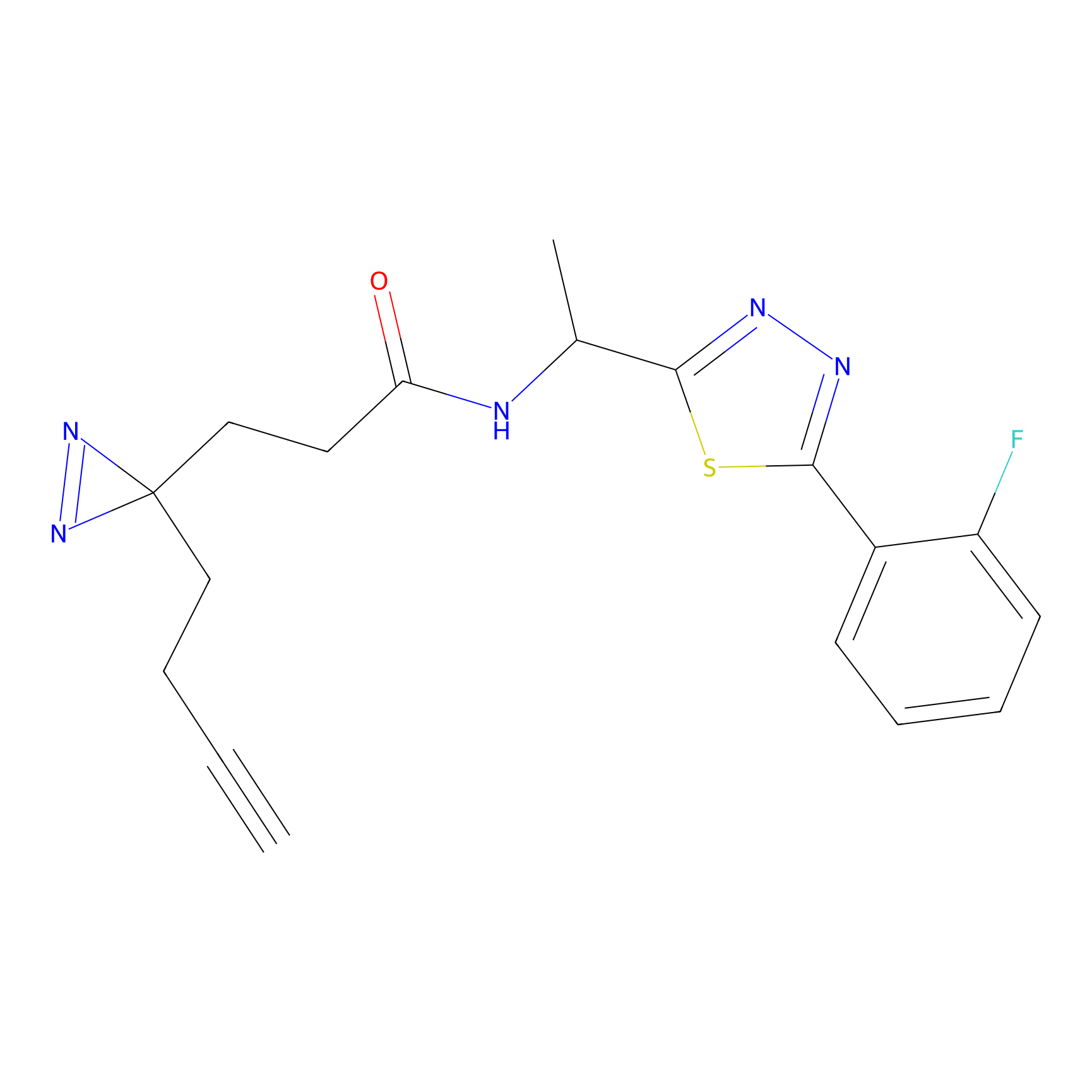
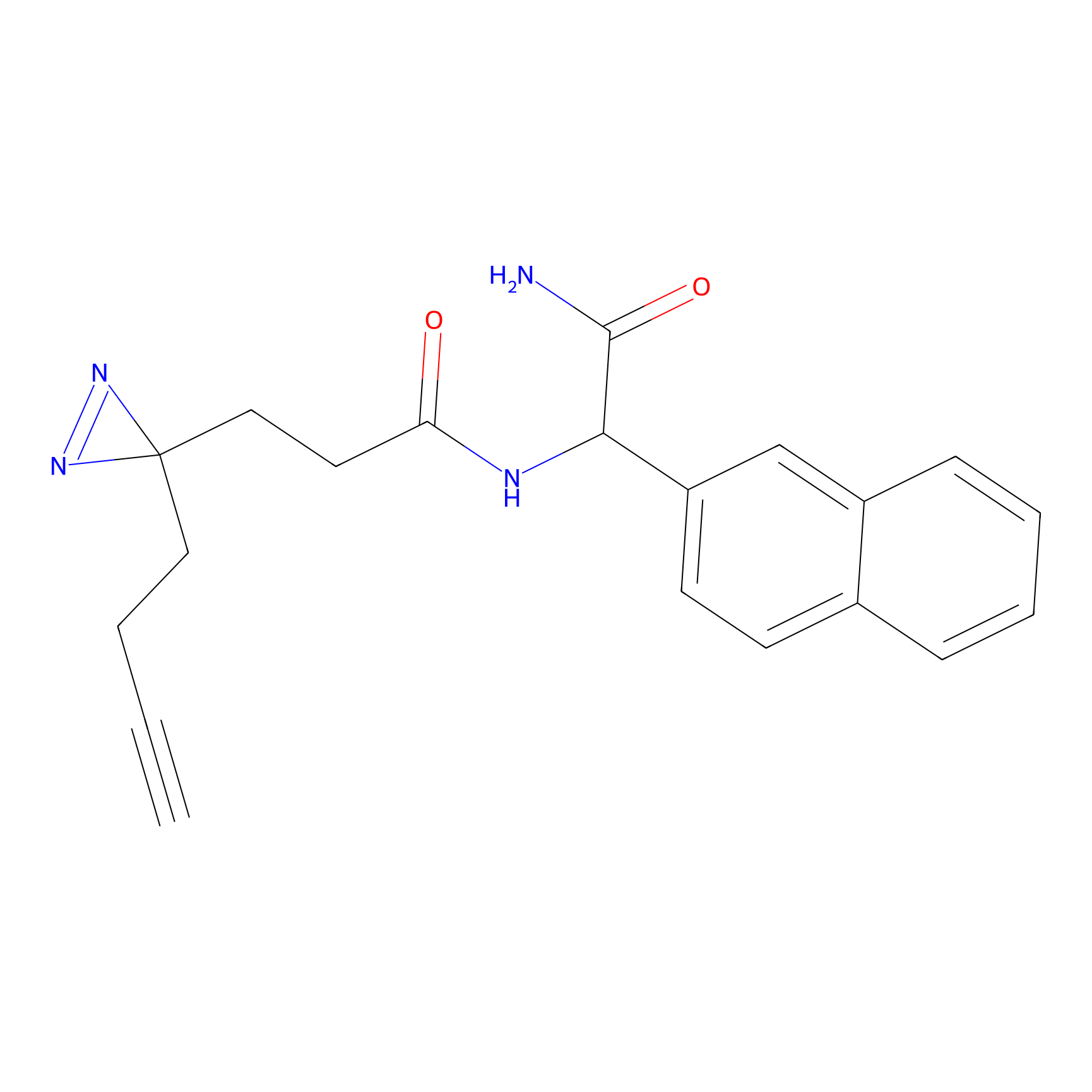
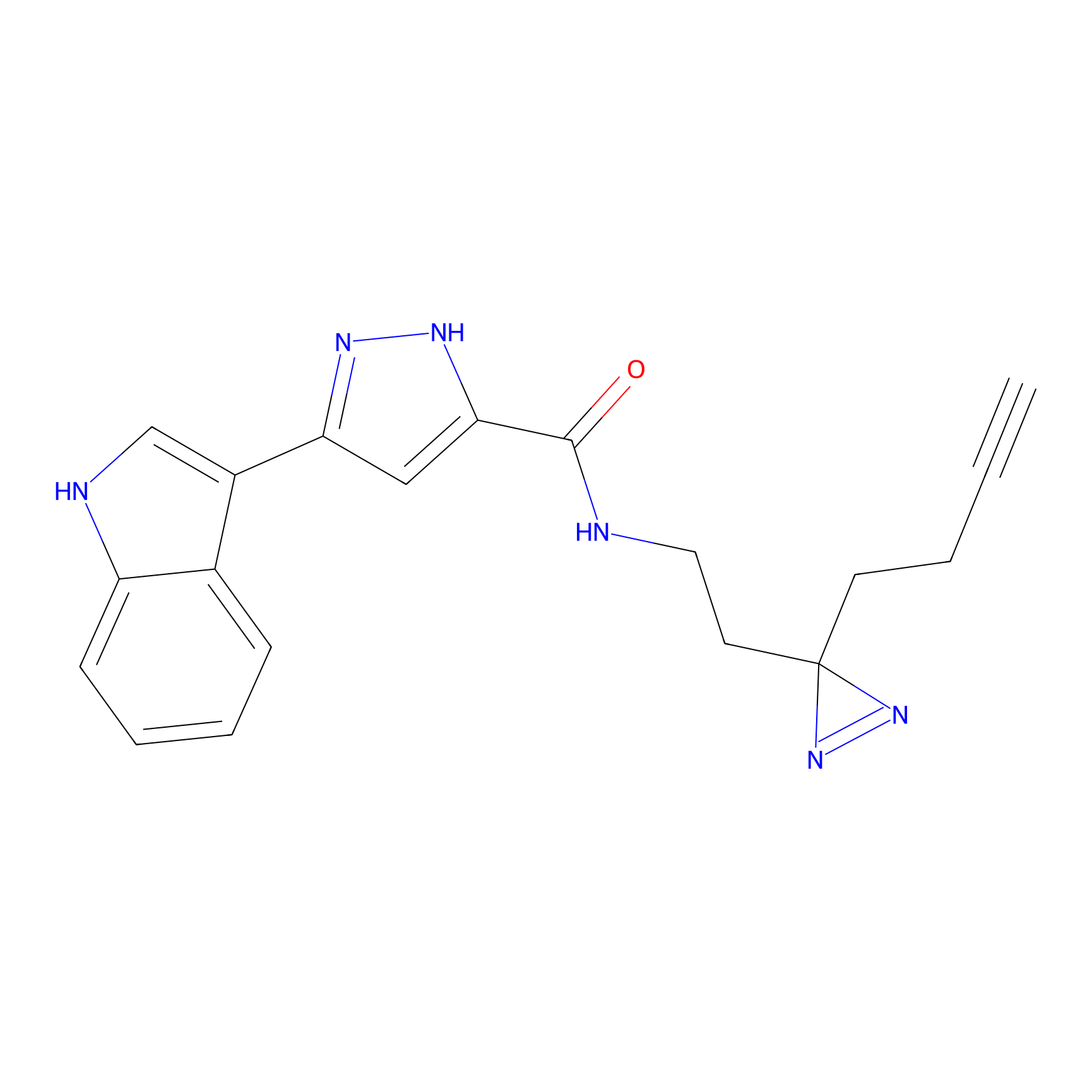
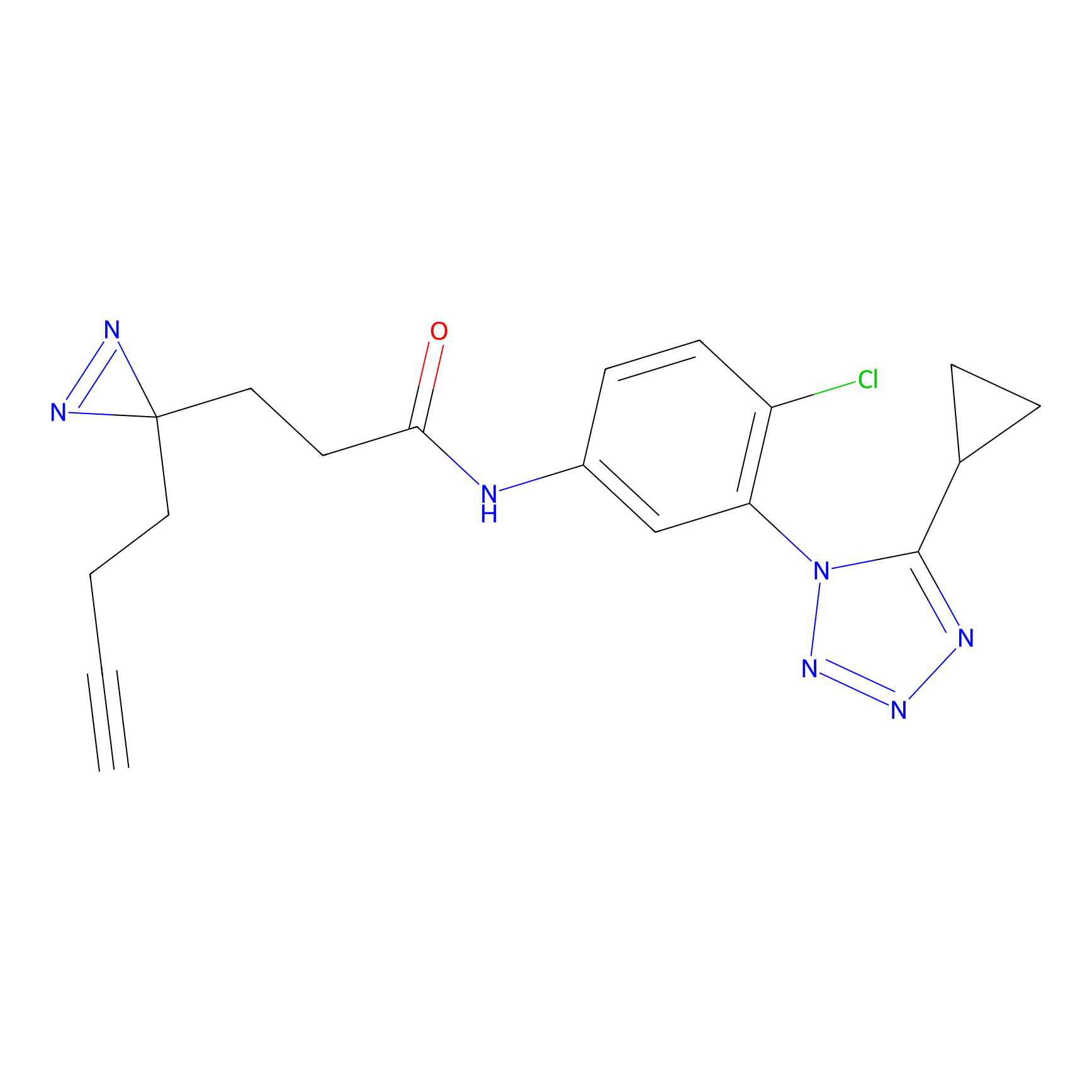
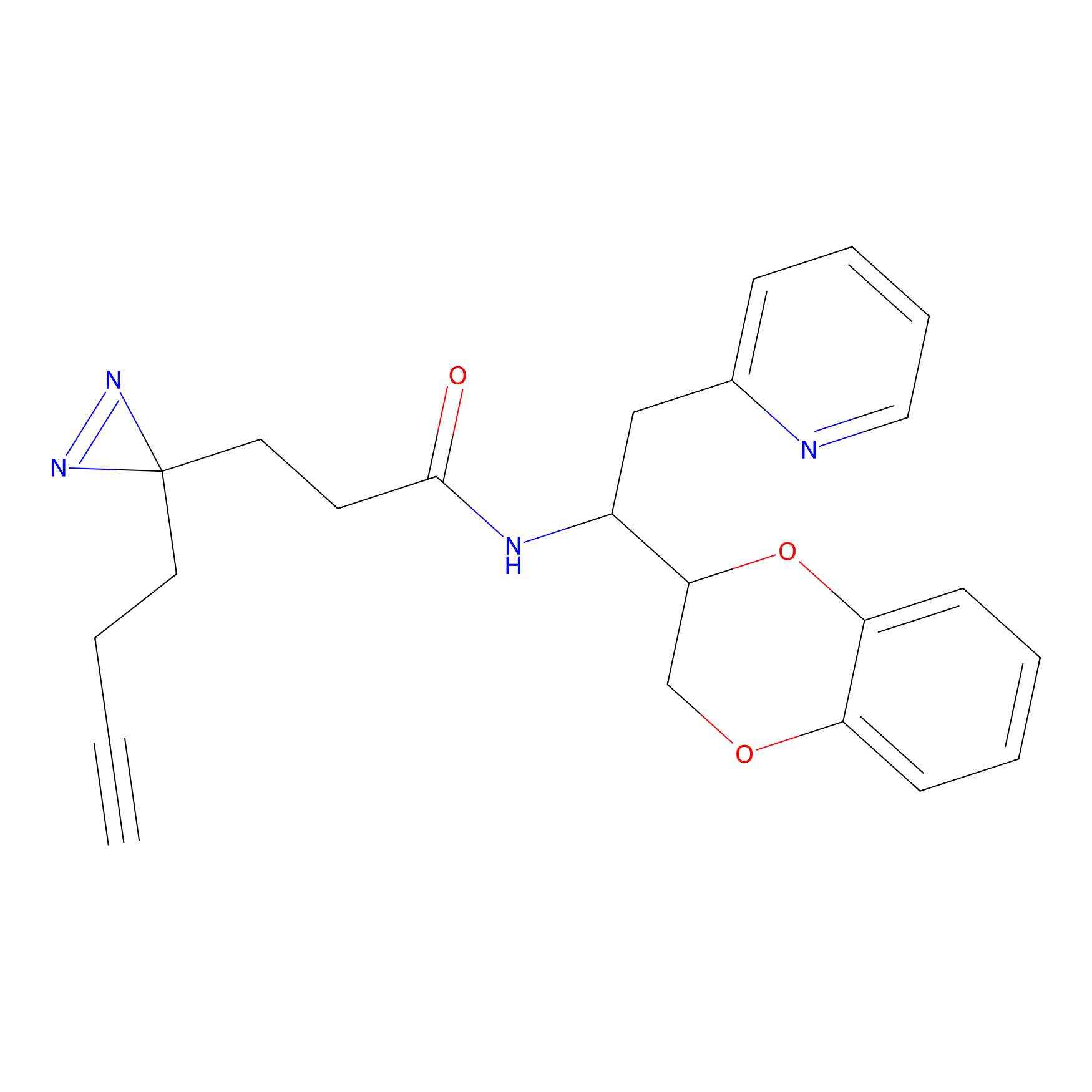
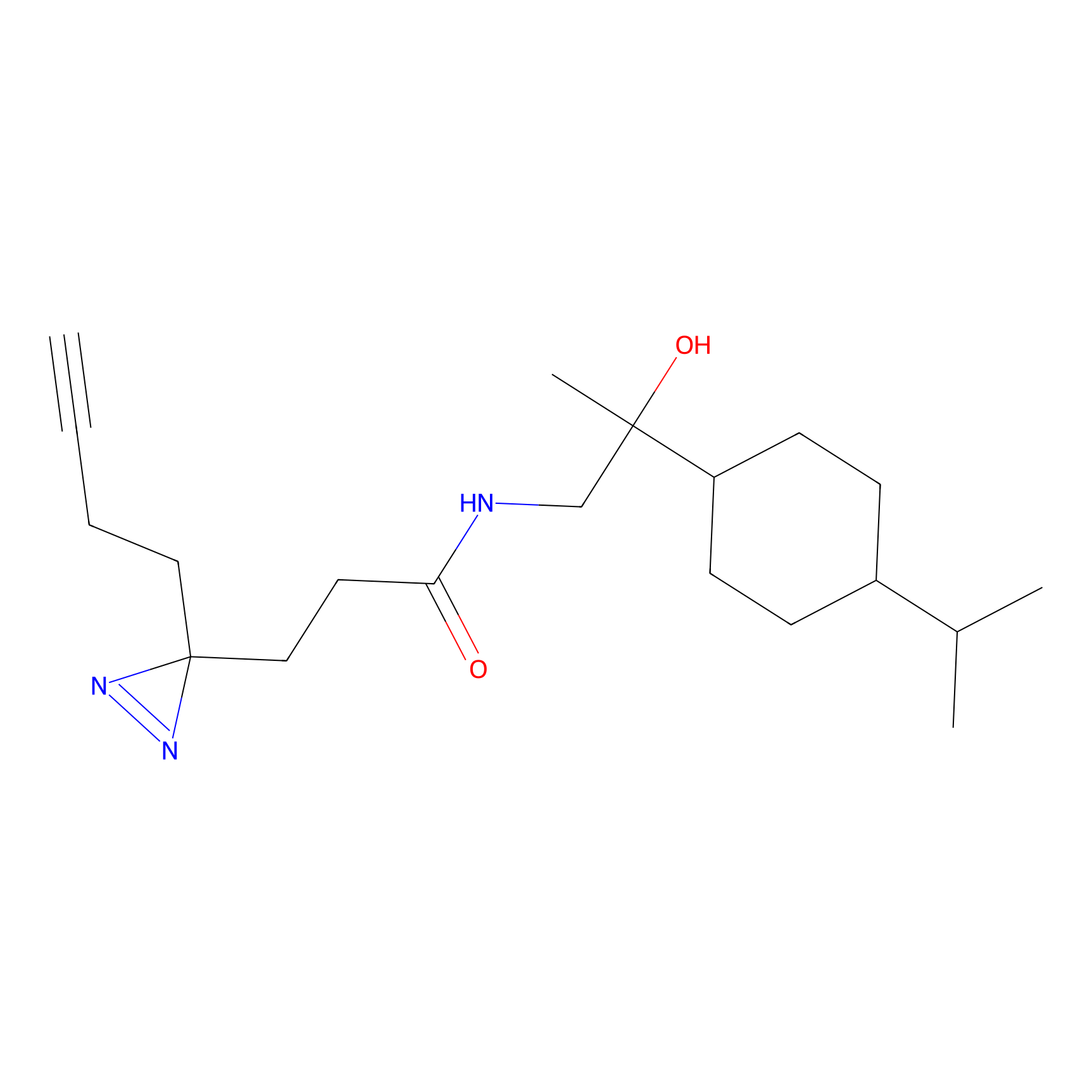
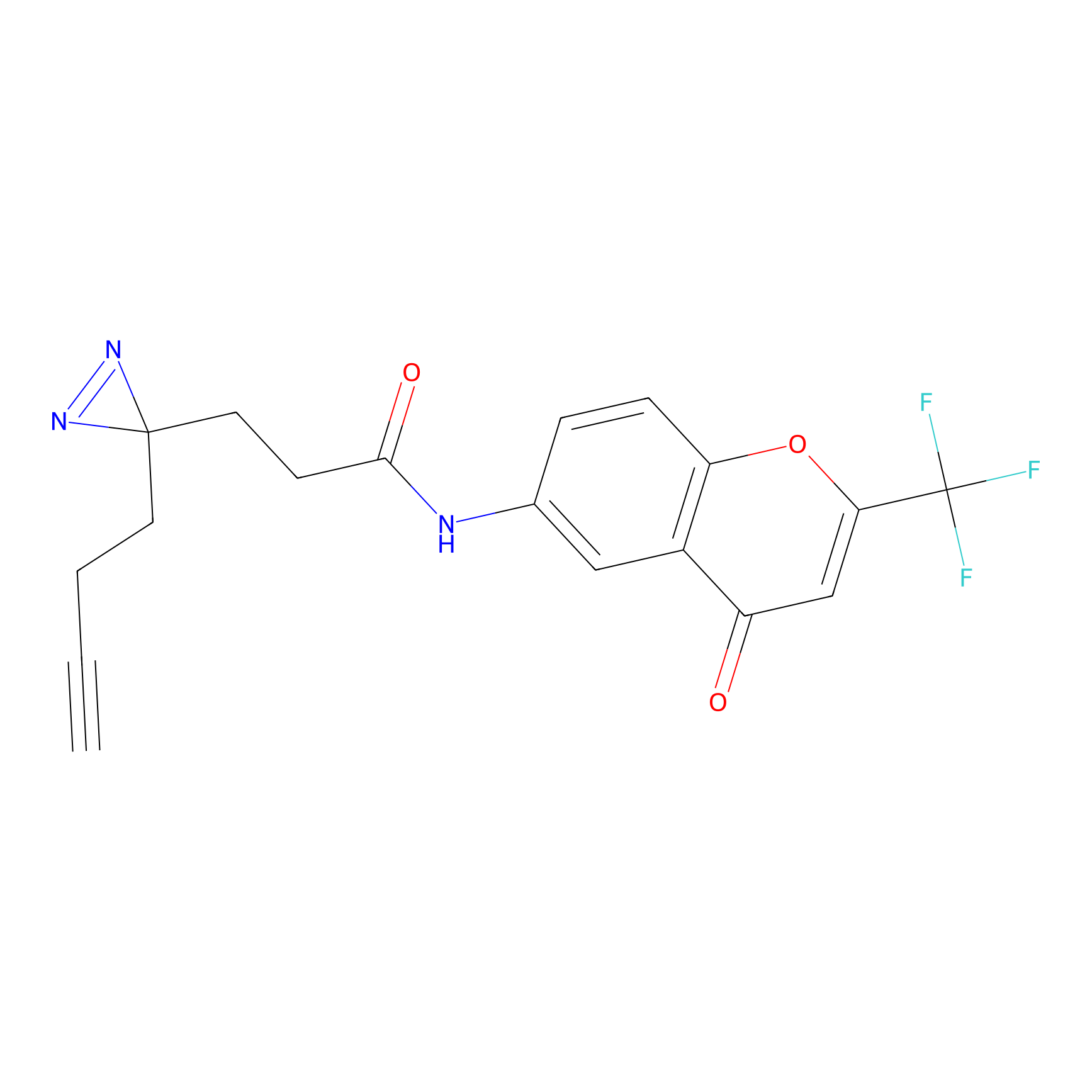
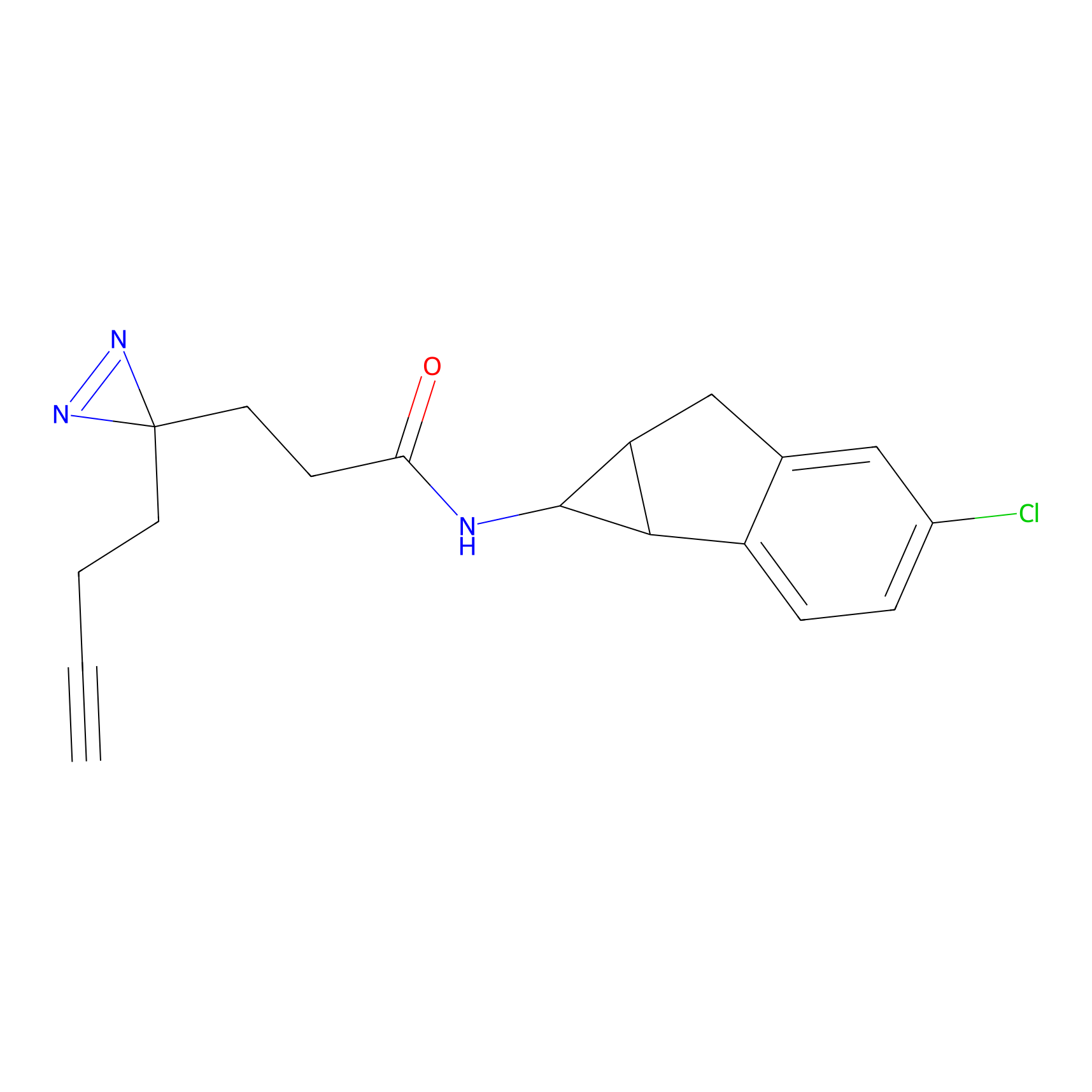
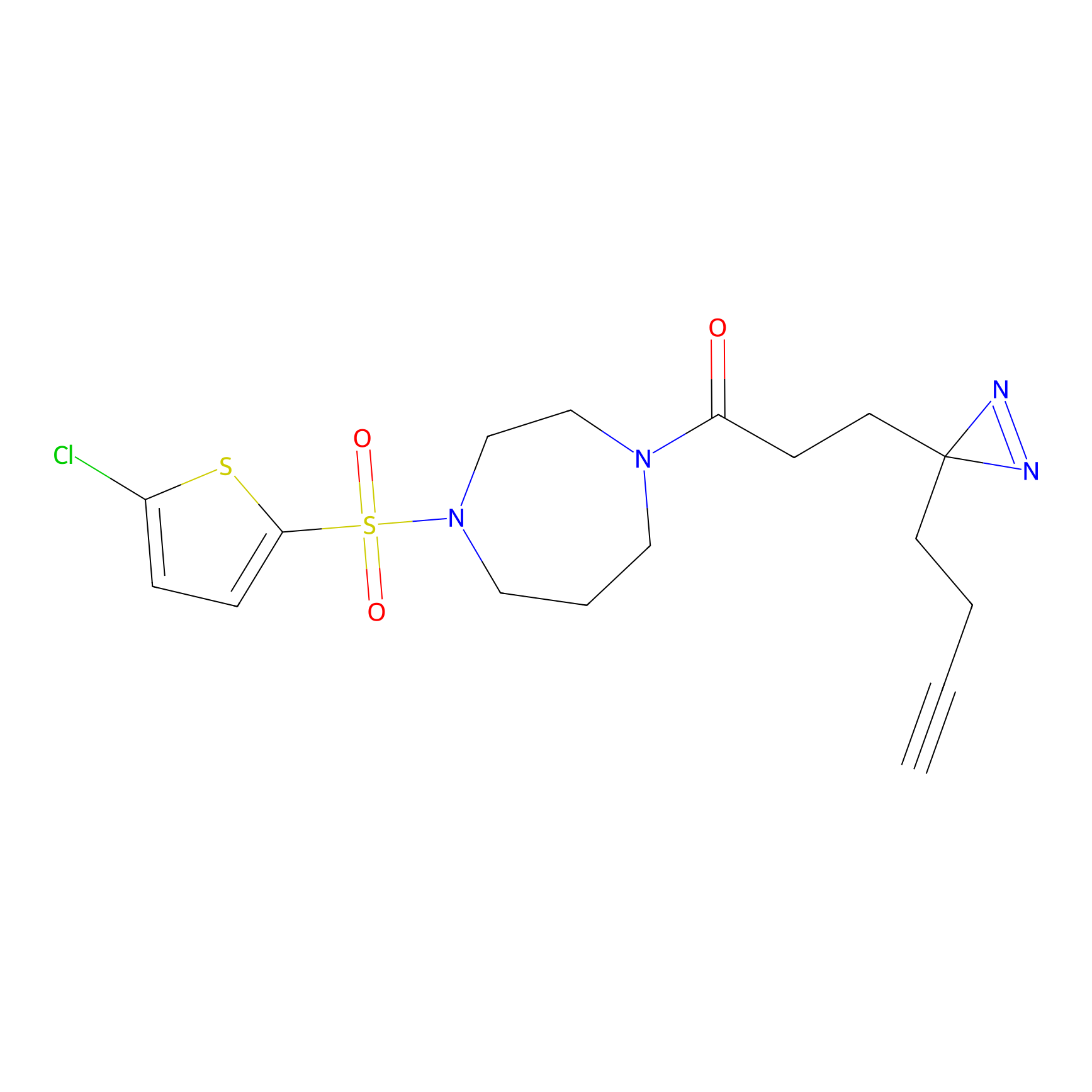
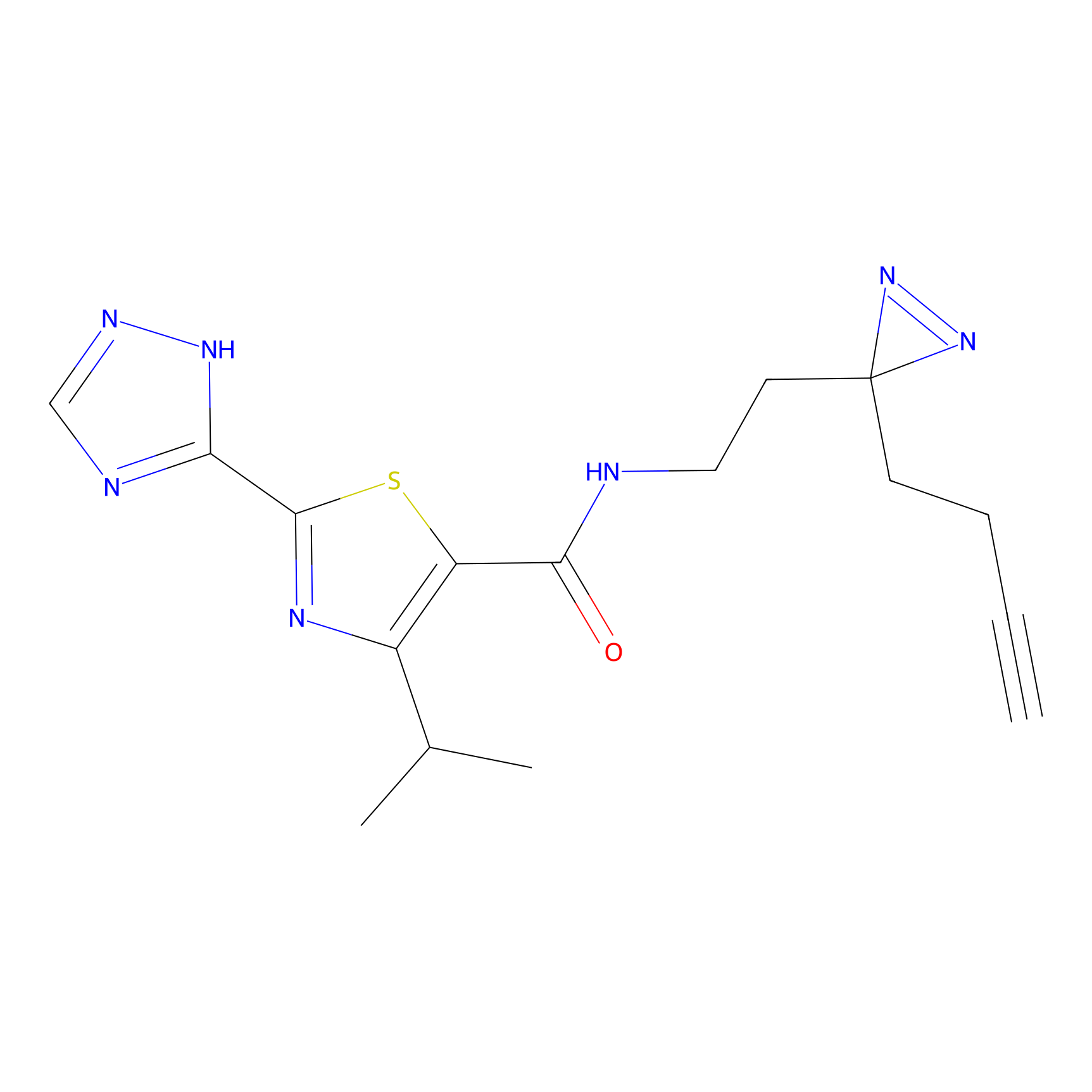
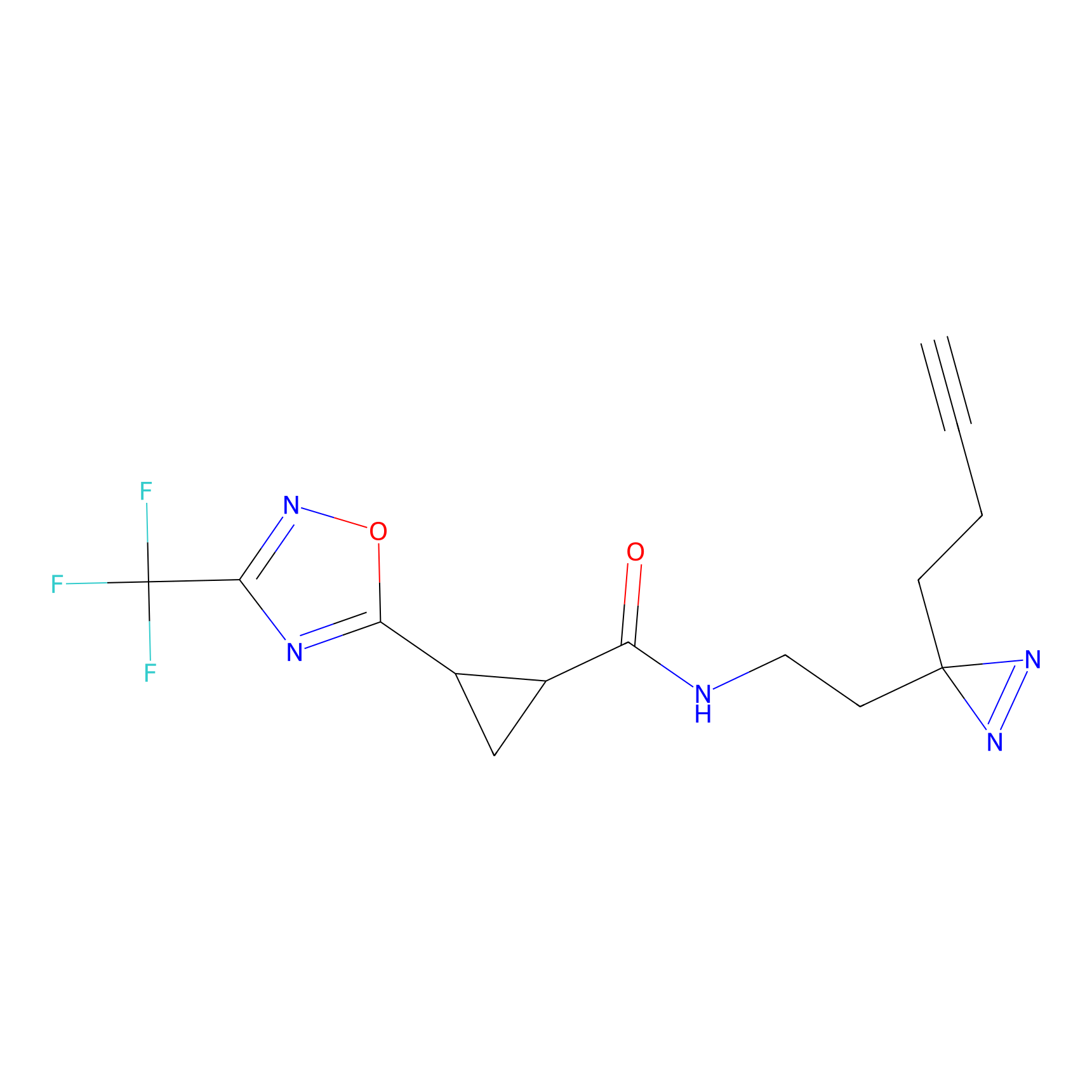
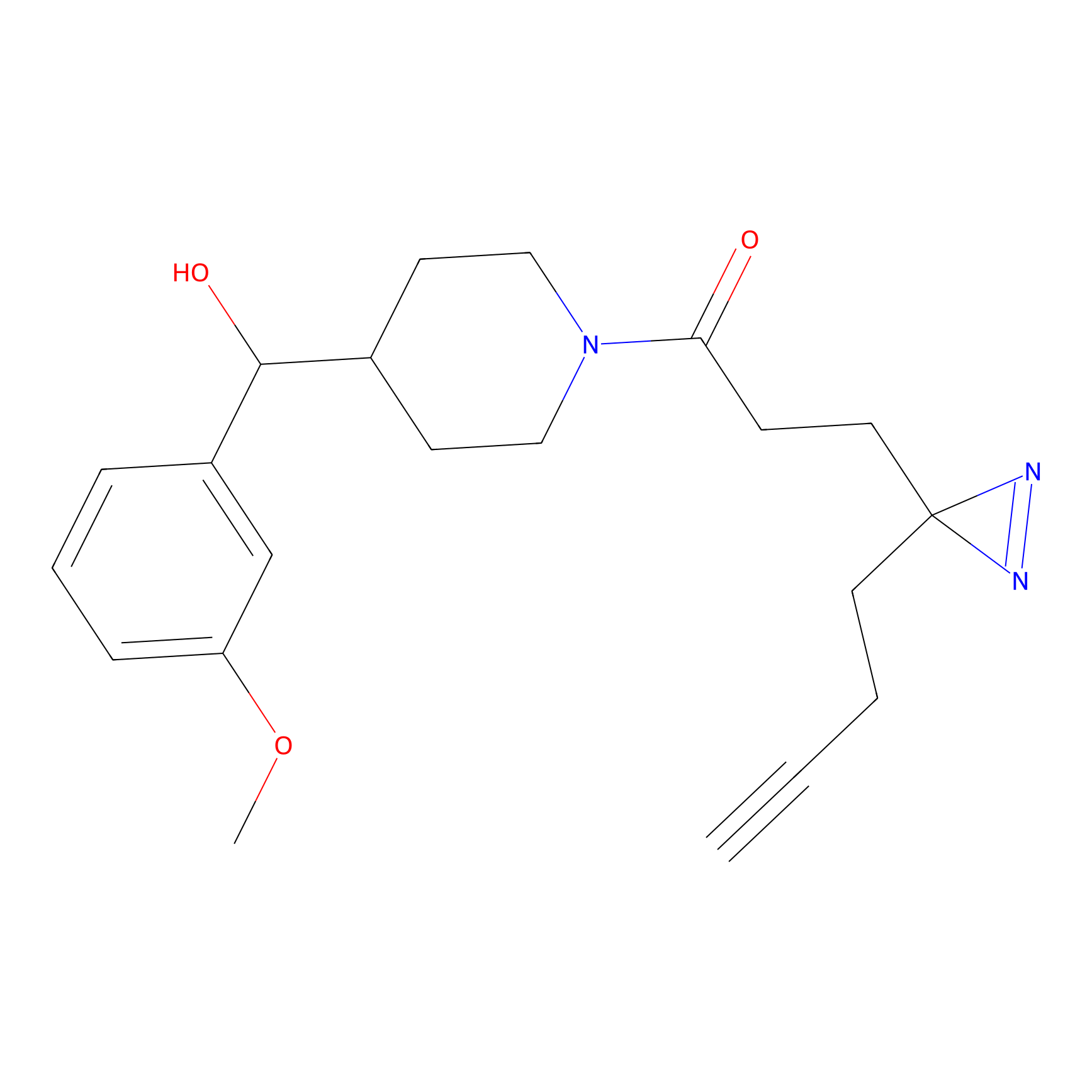
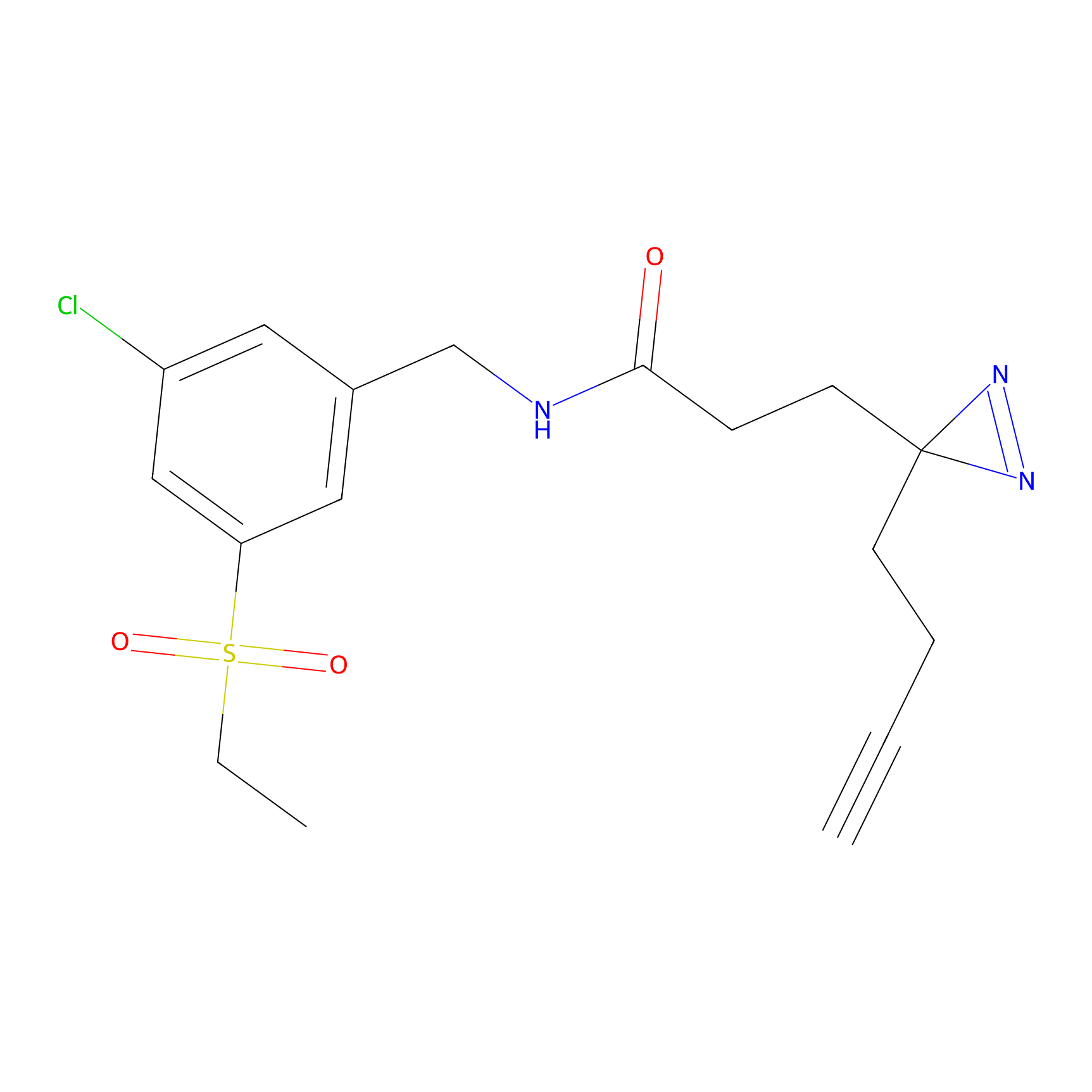
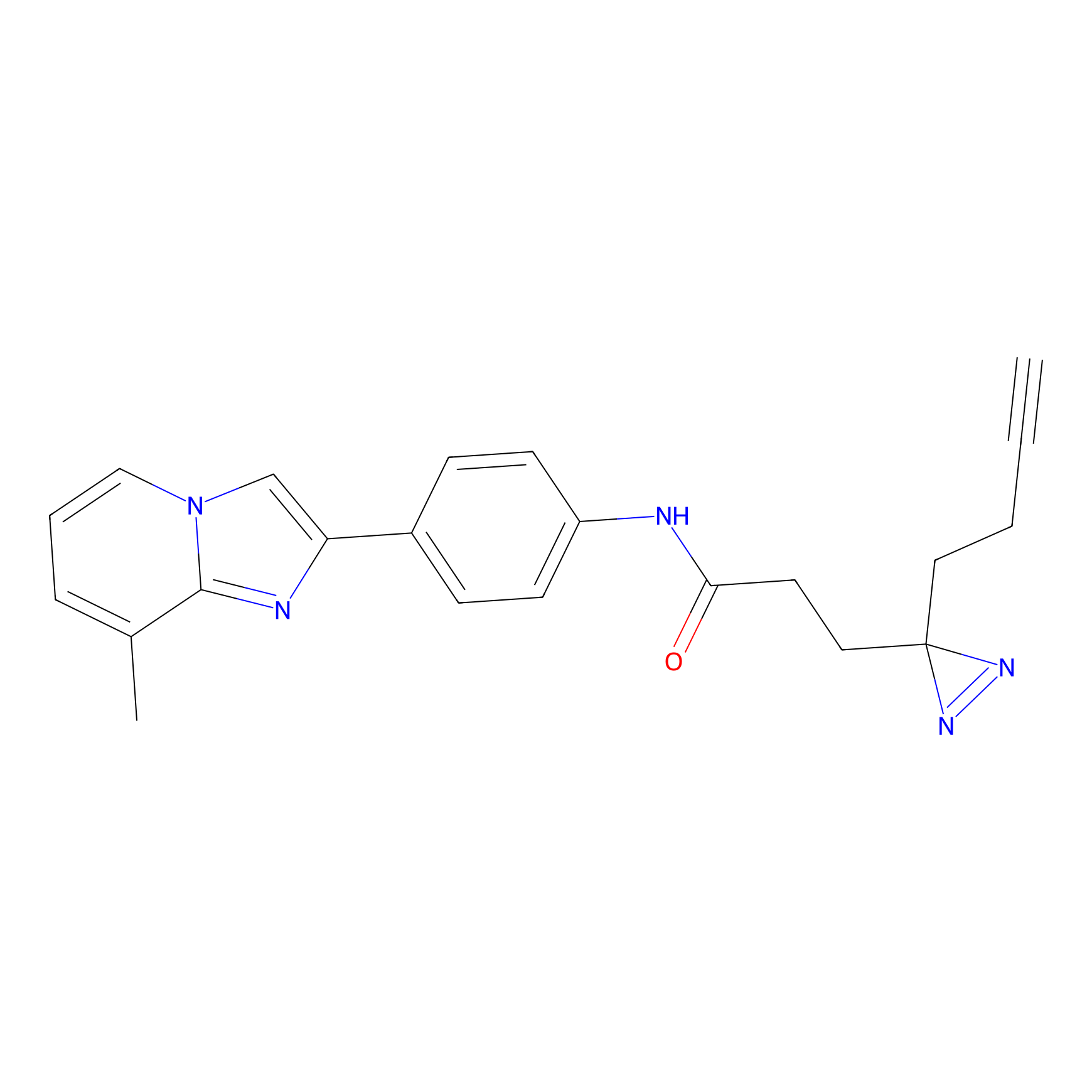
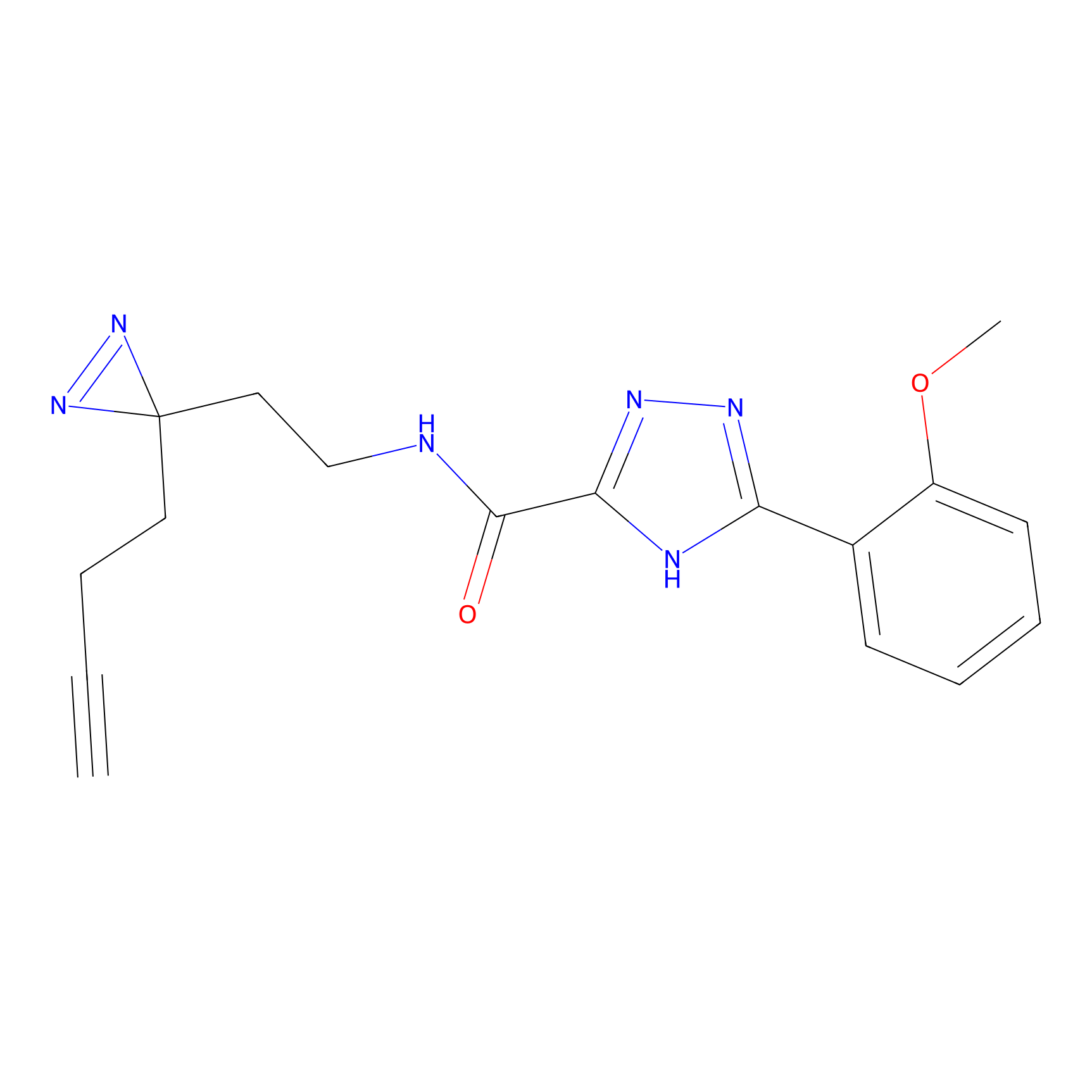
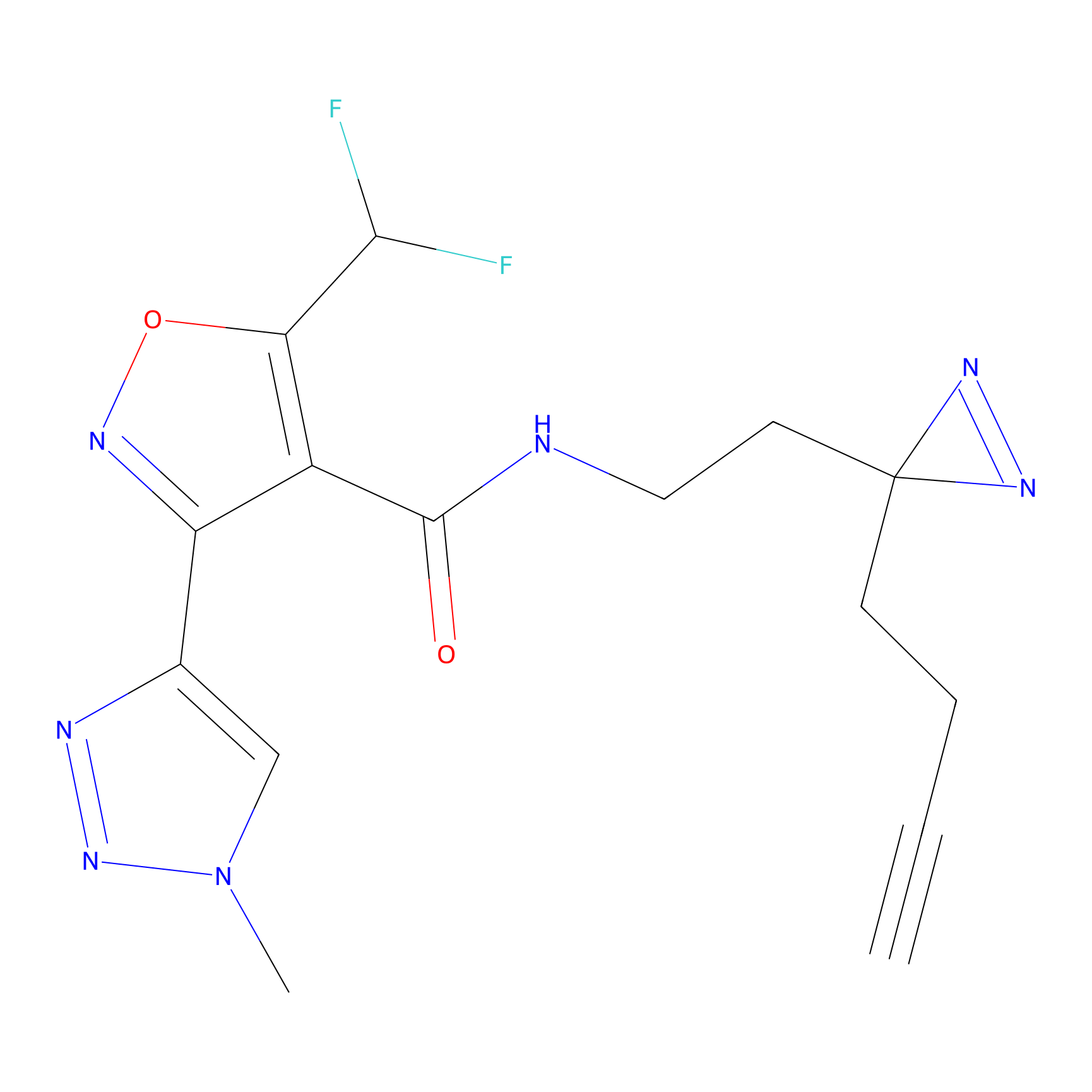
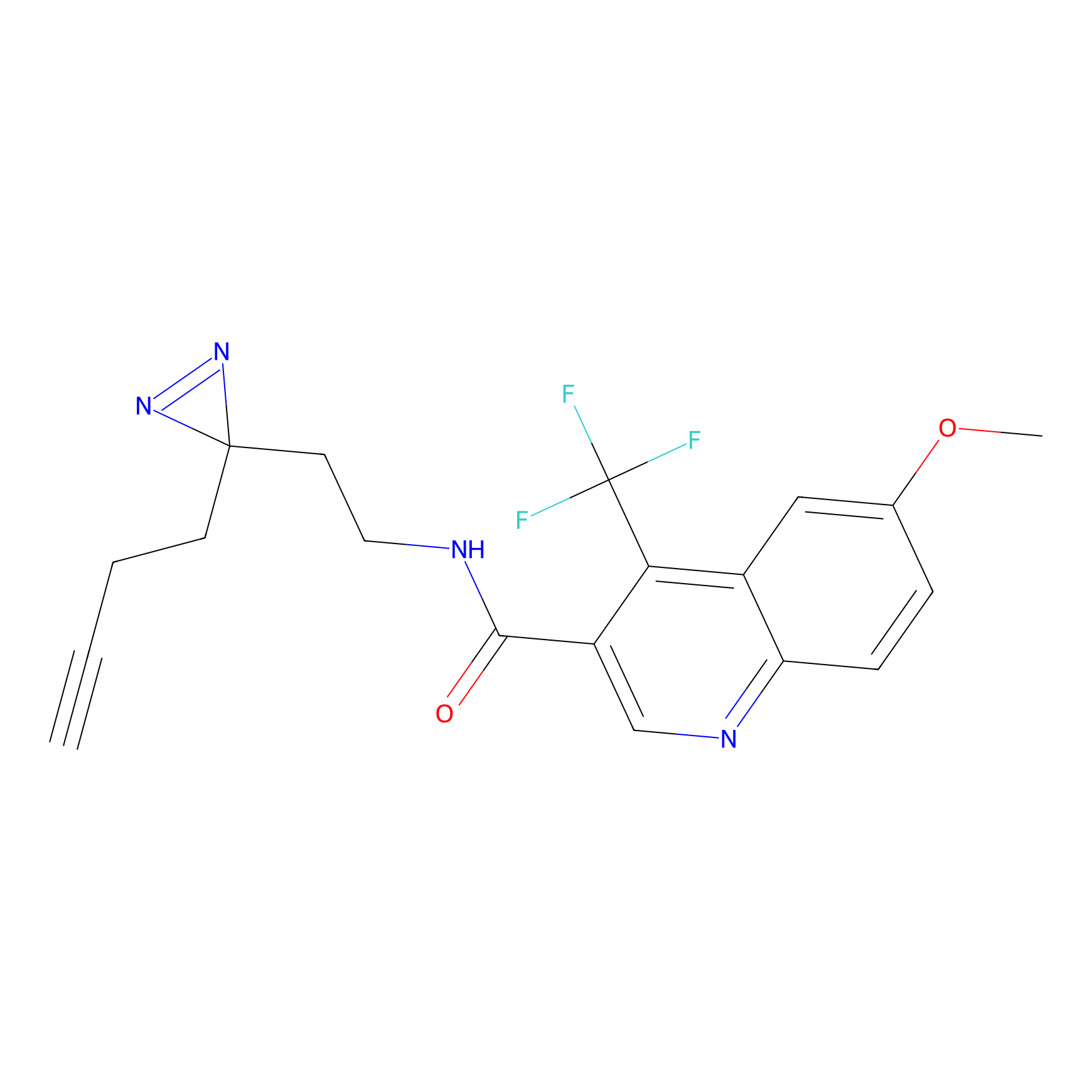
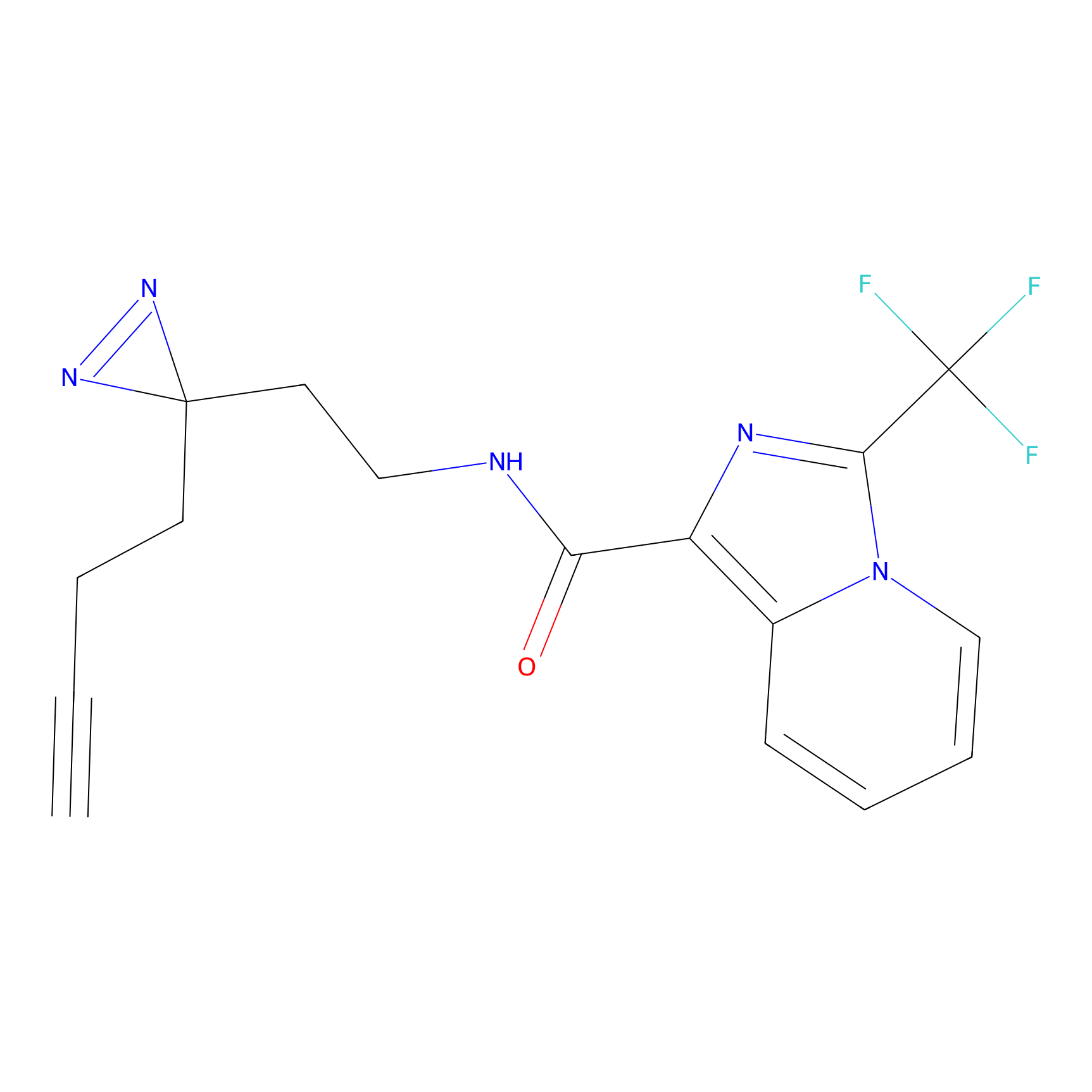
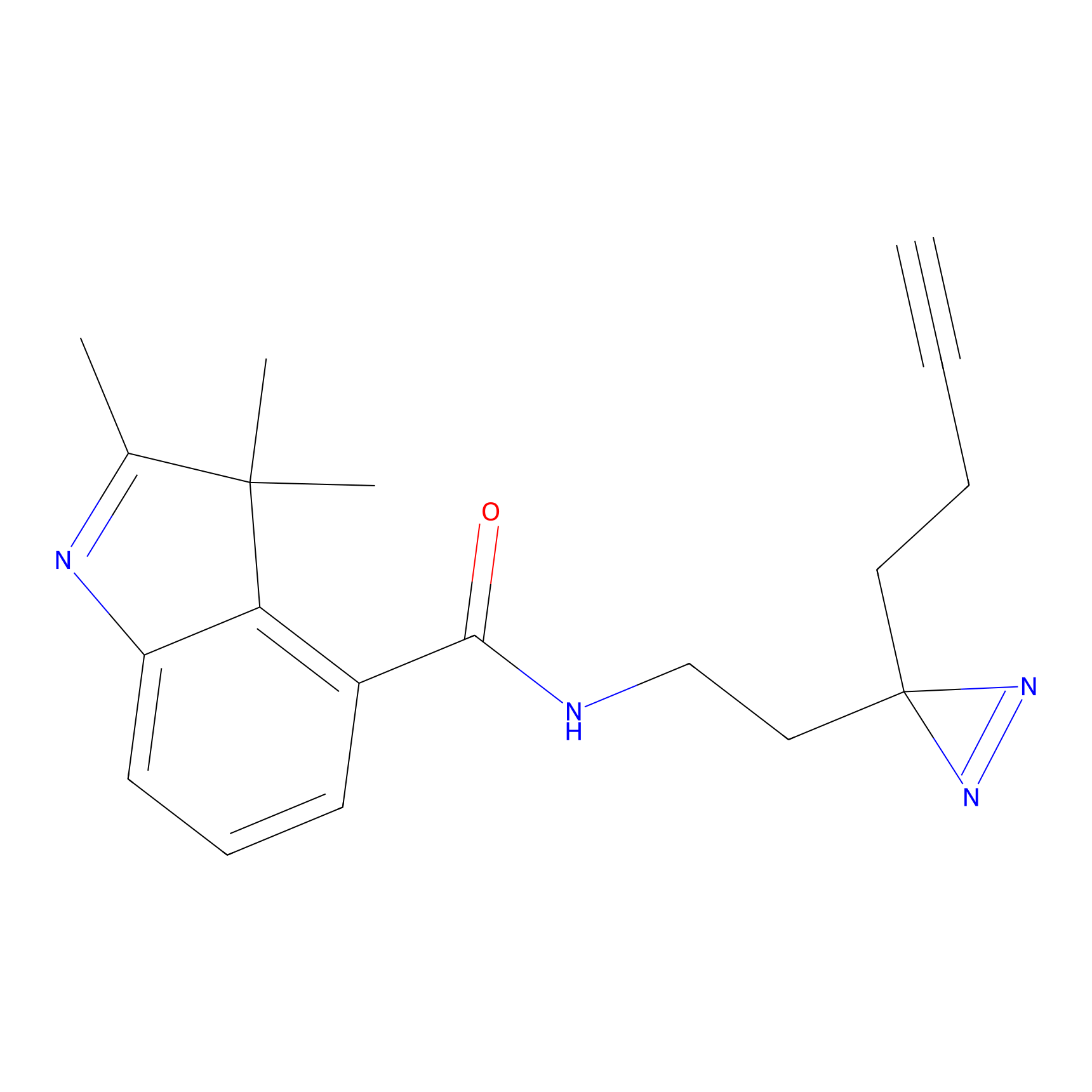
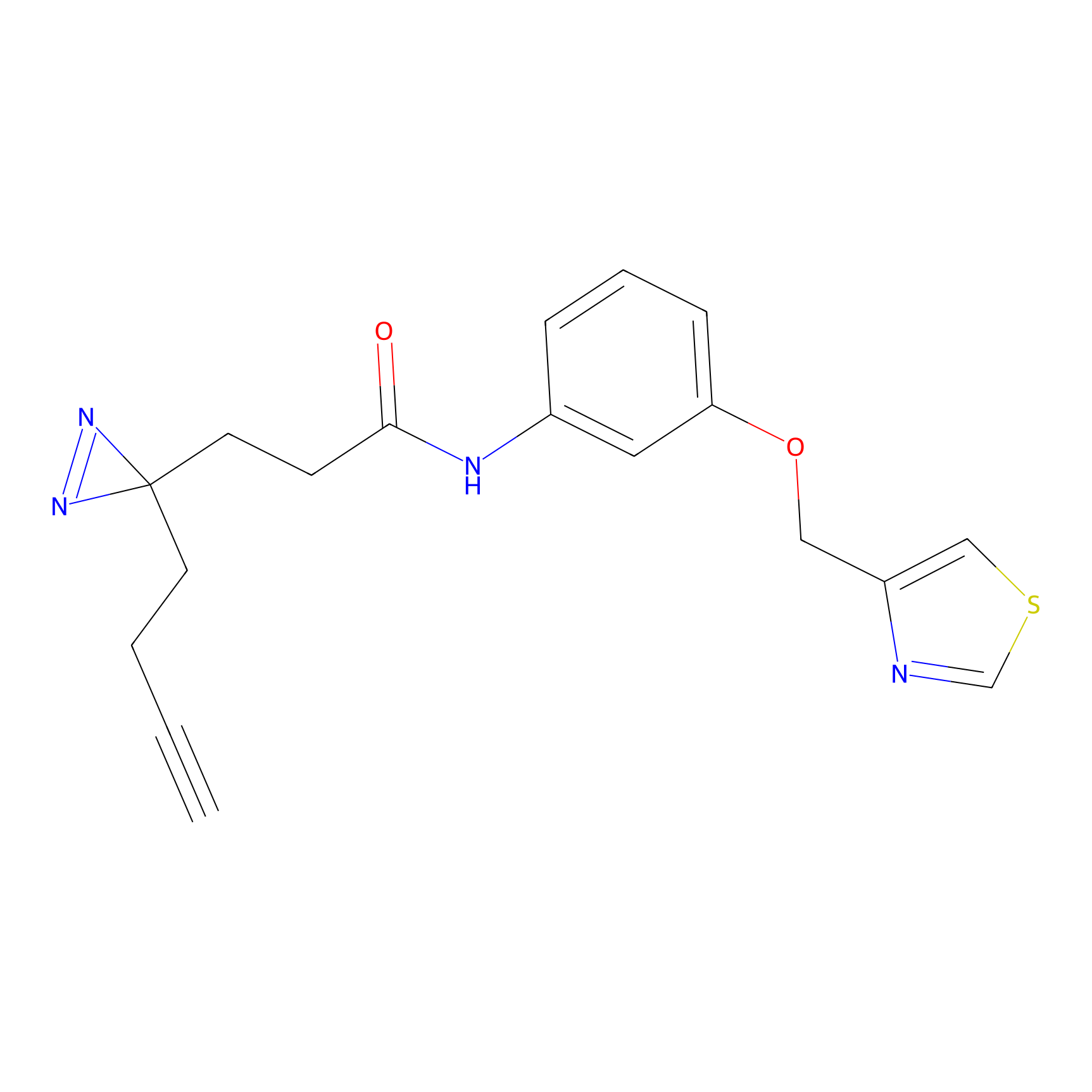
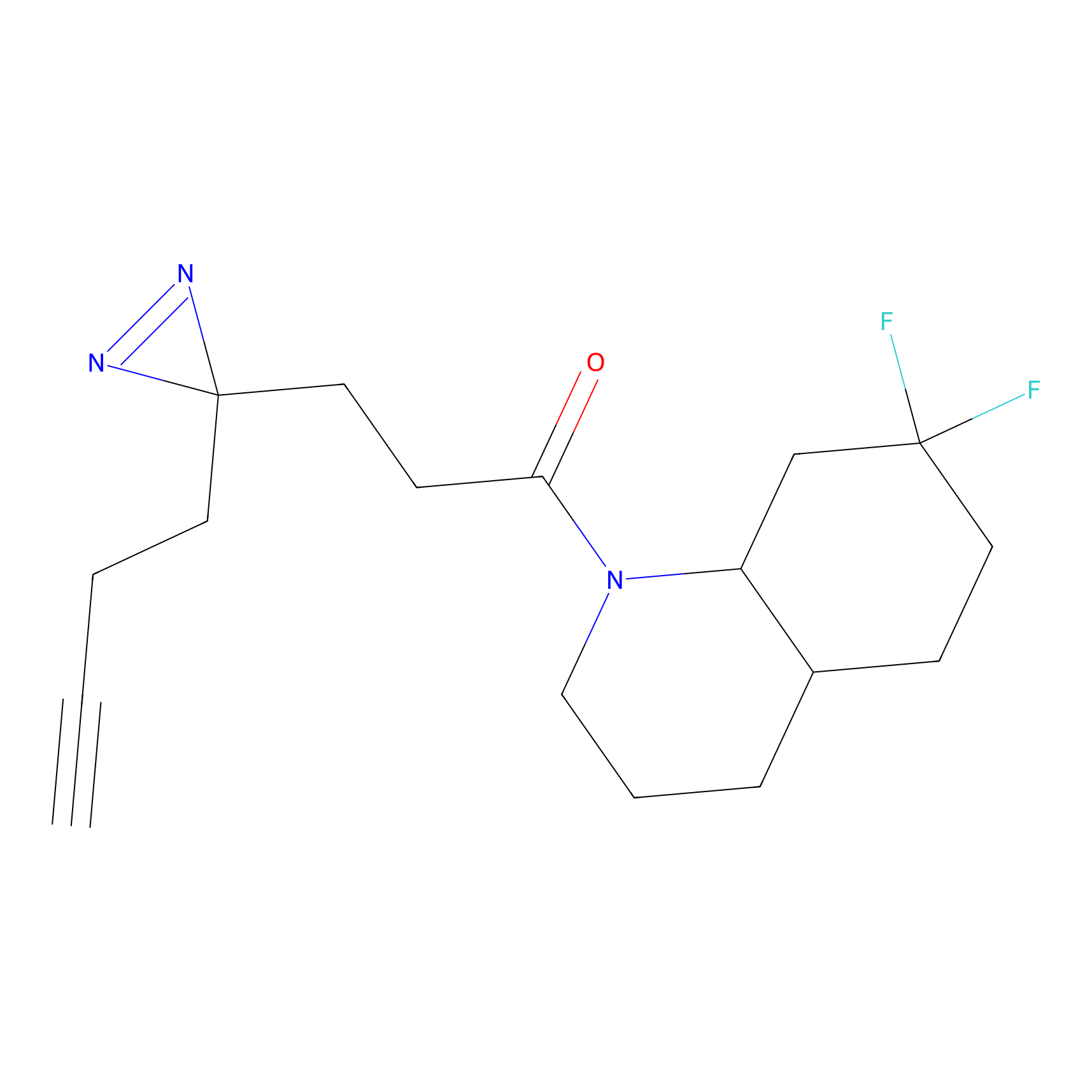
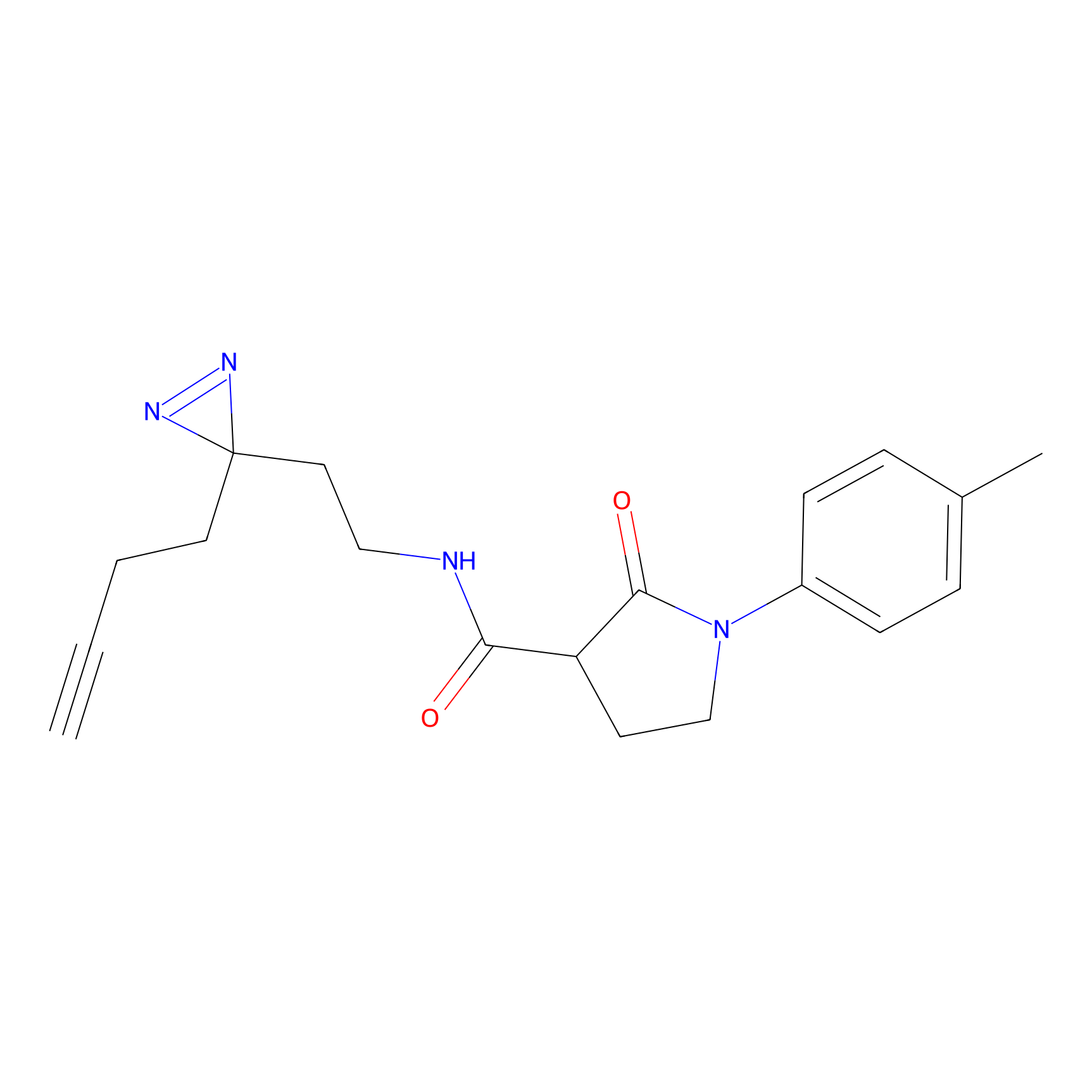
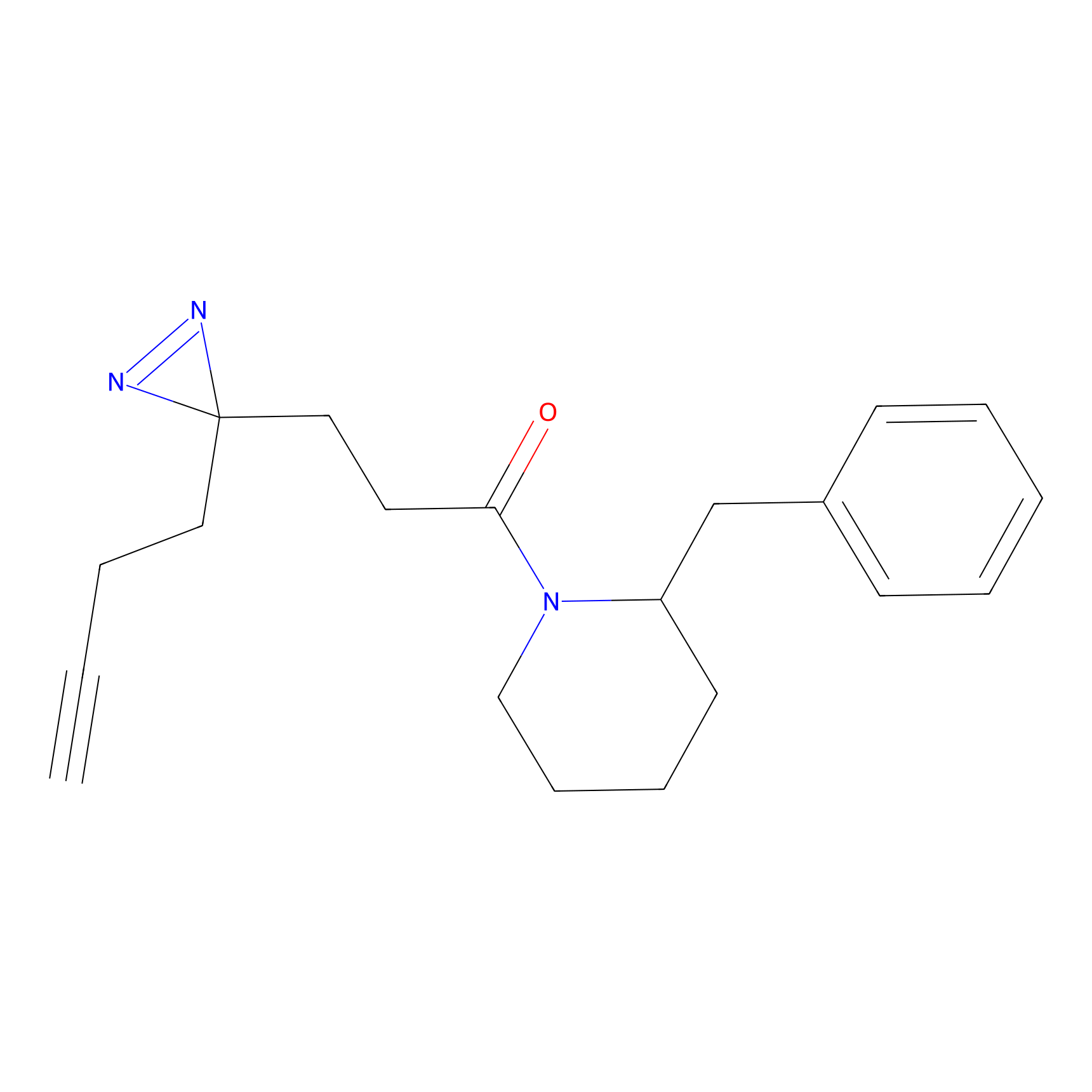
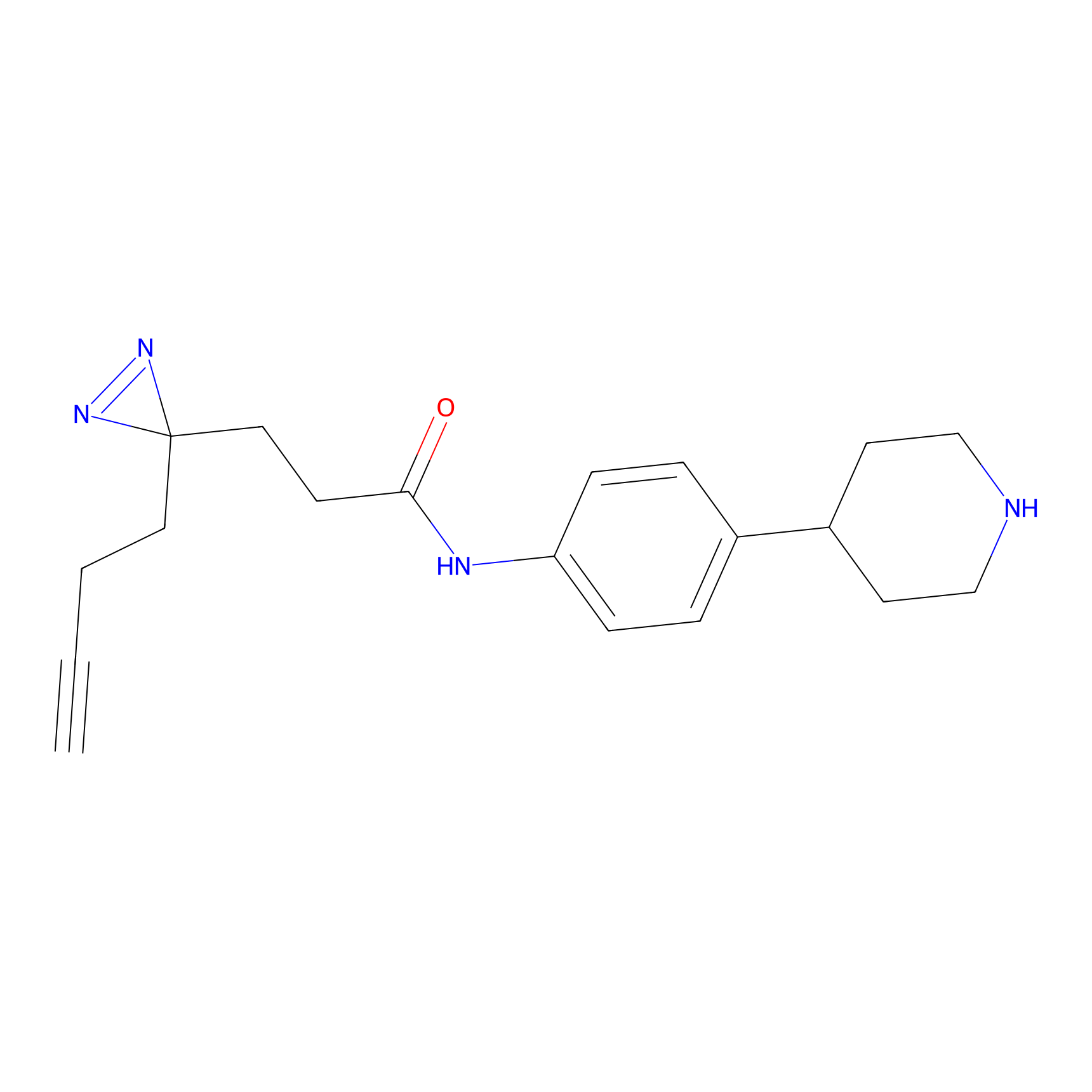
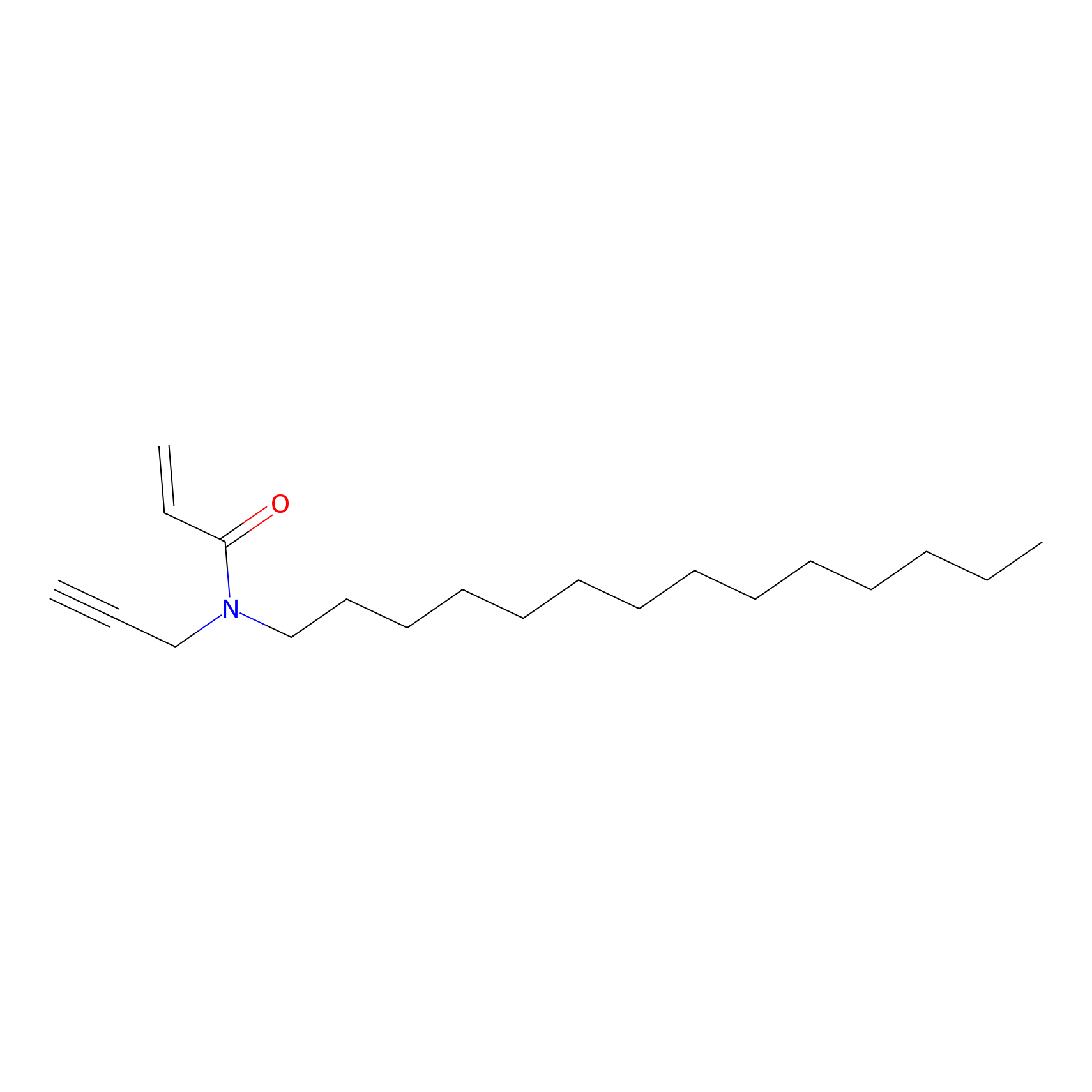
|
AOyne Probe Info |
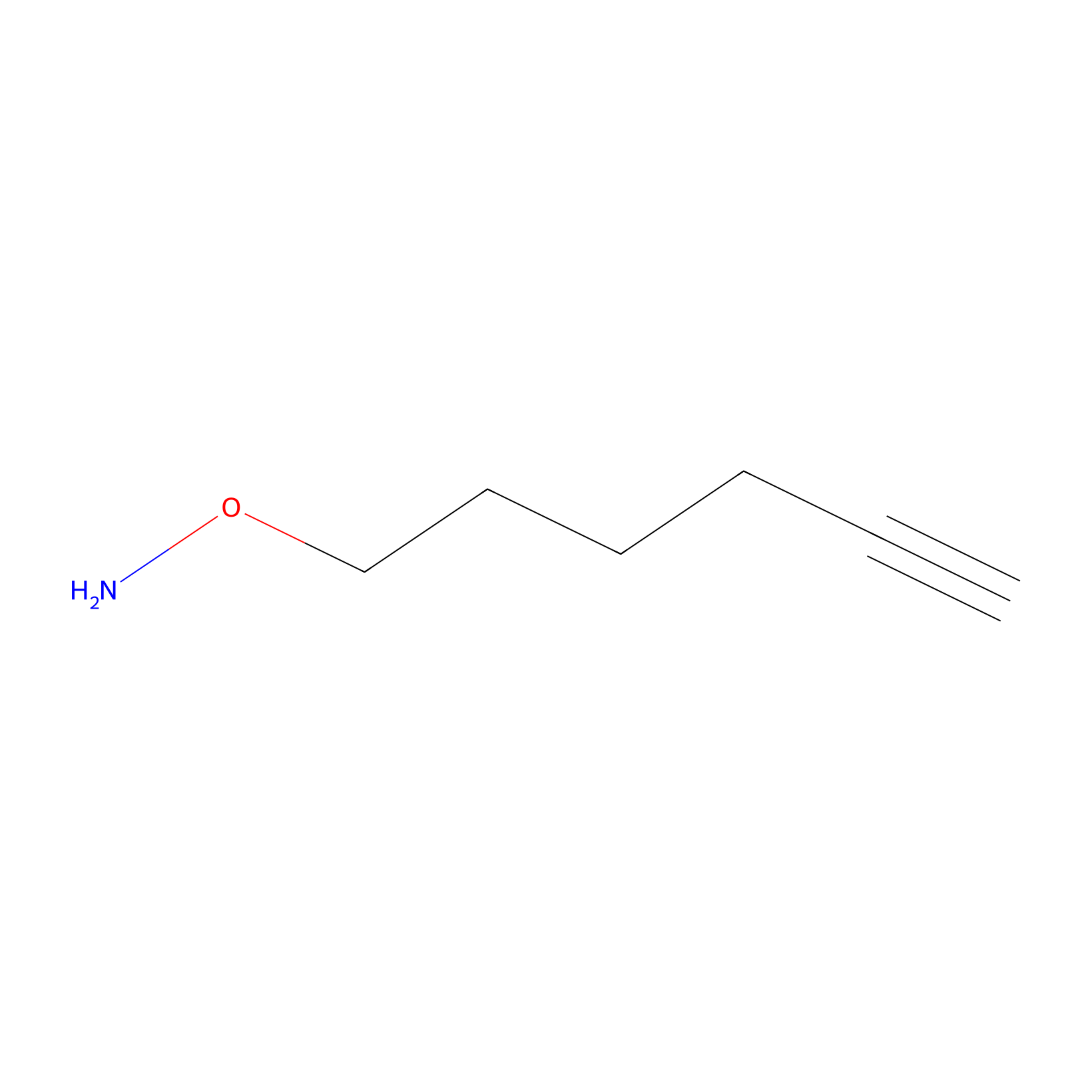 |
15.00 | LDD0443 | [3] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
The Interaction Atlas With This Target
References