Details of the Target
General Information of Target
| Target ID | LDTP17641 | |||||
|---|---|---|---|---|---|---|
| Target Name | Solute carrier family 35 member F2 (SLC35F2) | |||||
| Gene Name | SLC35F2 | |||||
| Gene ID | 54733 | |||||
| Synonyms |
Solute carrier family 35 member F2 |
|||||
| 3D Structure | ||||||
| Sequence |
MAVVIRLLGLPFIAGPVDIRHFFTGLTIPDGGVHIIGGEIGEAFIIFATDEDARRAISRS
GGFIKDSSVELFLSSKAEMQKTIEMKRTDRVGRGRPGSGTSGVDSLSNFIESVKEEASNS GYGSSINQDAGFHTNGTGHGNLRPRKTRPLKAENPYLFLRGLPYLVNEDDVRVFFSGLCV DGVIFLKHHDGRNNGDAIVKFASCVDASGGLKCHRSFMGSRFIEVMQGSEQQWIEFGGNA VKEGDVLRRSEEHSPPRGINDRHFRKRSHSKSPRRTRSRSPLGFYVHLKNLSLSIDERDL RNFFRGTDLTDEQIRFLYKDENRTRYAFVMFKTLKDYNTALSLHKTVLQYRPVHIDPISR KQMLKFIARYEKKRSGSLERDRPGHVSQKYSQEGNSGQKLCIYIRNFPFDVTKVEVQKFF ADFLLAEDDIYLLYDDKGVGLGEALVKFKSEEQAMKAERLNRRRFLGTEVLLRLISEAQI QEFGVNFSVMSSEKMQARSQSRERGDHSHLFDSKDPPIYSVGAFENFRHQLEDLRQLDNF KHPQRDFRQPDRHPPEDFRHSSEDFRFPPEDFRHSPEDFRRPREEDFRRPSEEDFRRPWE EDFRRPPEDDFRHPREEDWRRPLEEDWRRPLEEDFRRSPTEDFRQLPEEDFRQPPEEDLR WLPEEDFRRPPEEDWRRPPEEDFRRPLQGEWRRPPEDDFRRPPEEDFRHSPEEDFRQSPQ EHFRRPPQEHFRRPPPEHFRRPPPEHFRRPPPEHFRRPPPEHFRRPPPEHFRRPPPEHFR RPPQEHFRRPPQEHFRRSREEDFRHPPDEDFRGPPDEDFRHPPDEDFRSPQEEDFRCPSD EDFRQLPEEDLREAPEEDPRLPDNFRPPGEDFRSPPDDFRSHRPFVNFGRPEGGKFDFGK HNMGSFPEGRFMPDPKINCGSGRVTPIKIMNLPFKANVNEILDFFHGYRIIPDSVSIQYN EQGLPTGEAIVAMINYNEAMAAIKDLNDRPVGPRKVKLTLL |
|||||
| Target Bioclass |
Transporter and channel
|
|||||
| Family |
SLC35F solute transporter family
|
|||||
| Subcellular location |
Membrane
|
|||||
| Function | Putative solute transporter. | |||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Target Site Mutations in Different Cell Lines
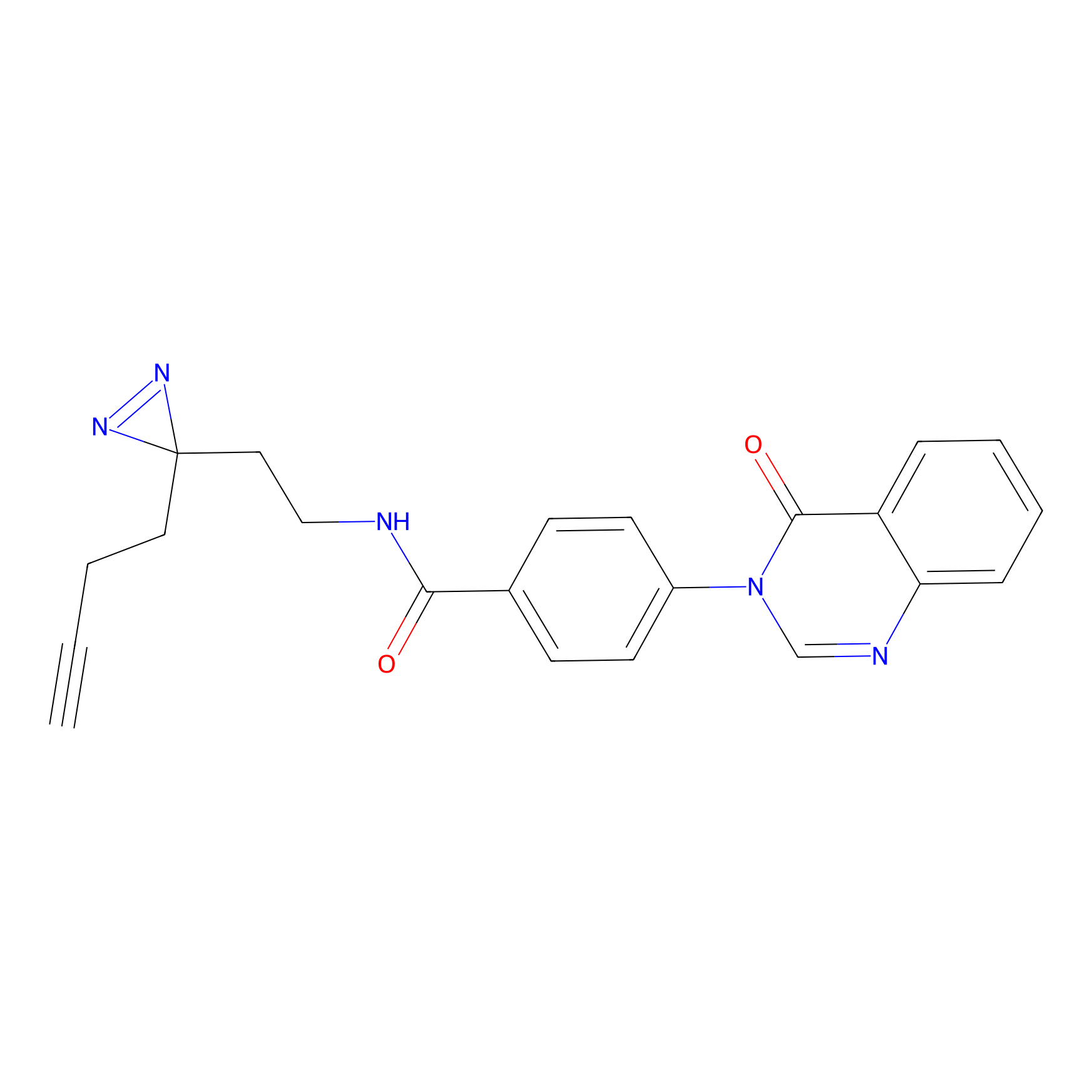
Probe(s) Labeling This Target
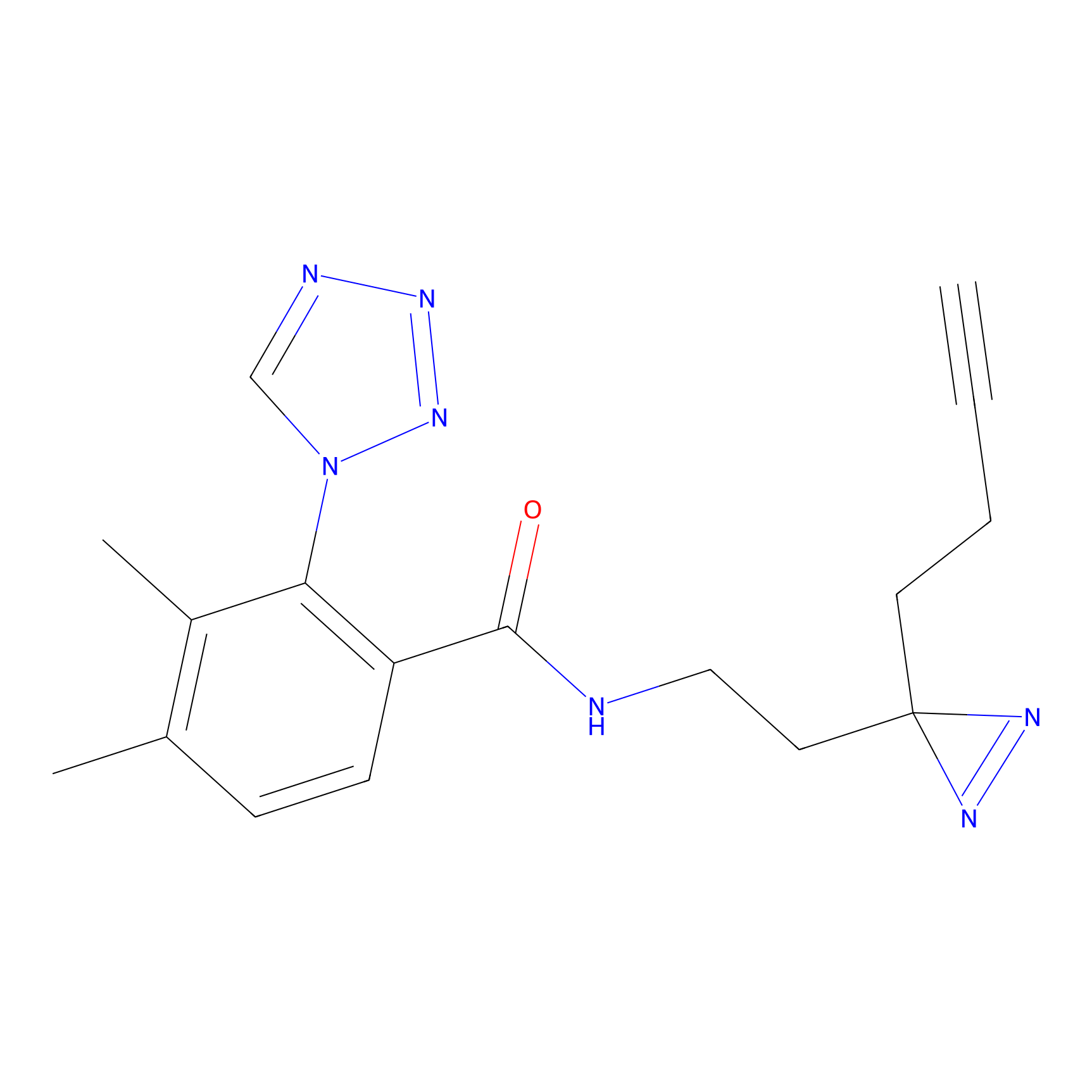
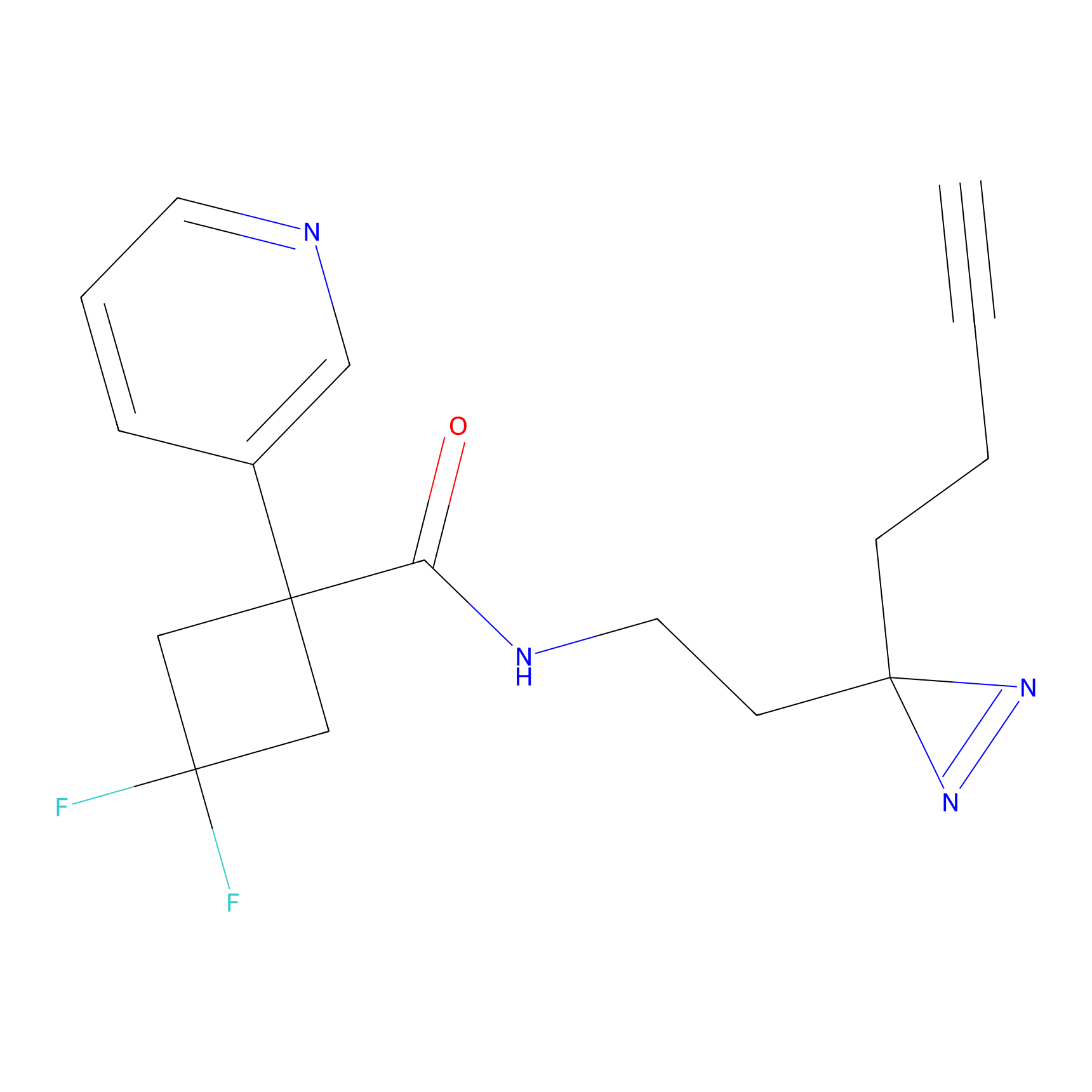
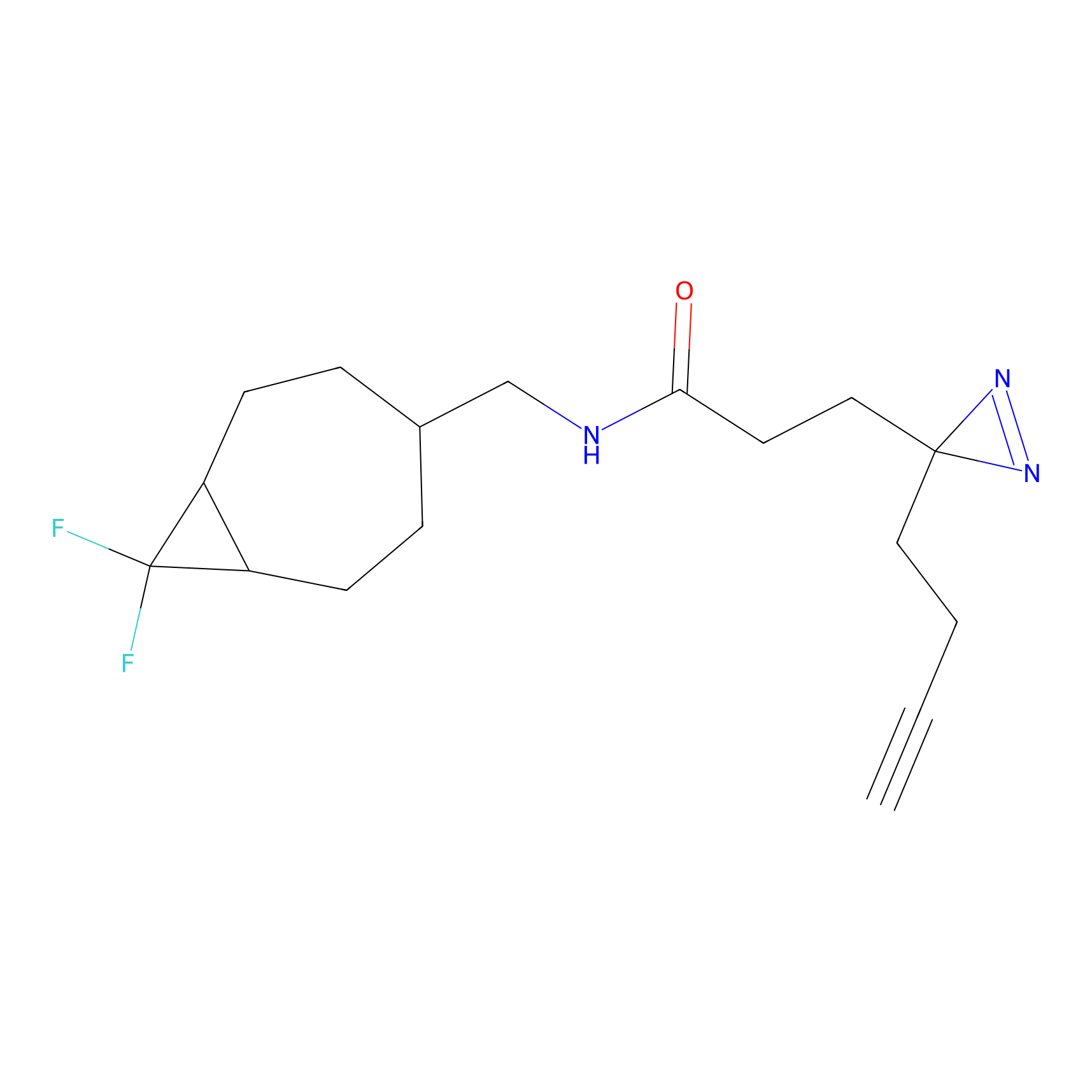
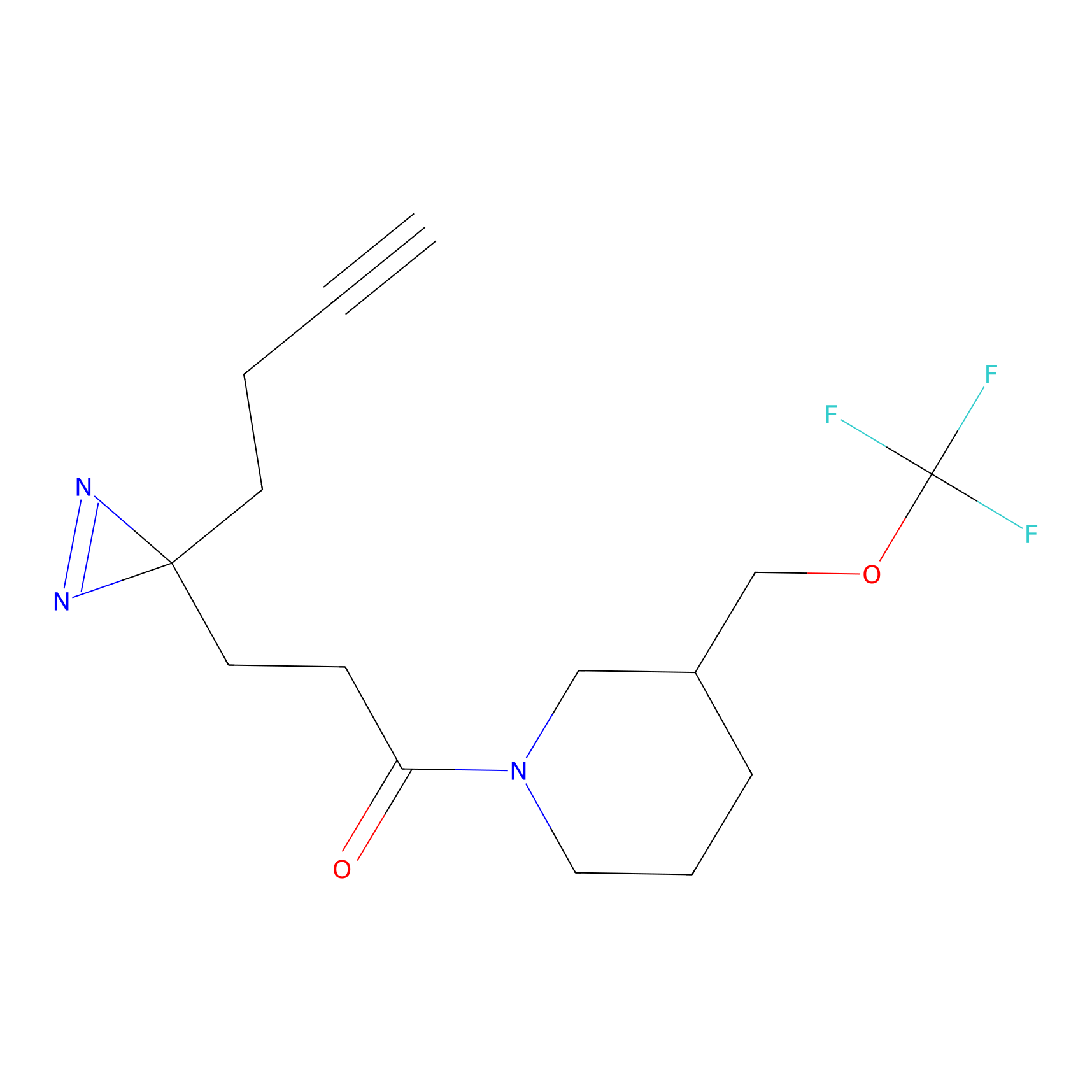
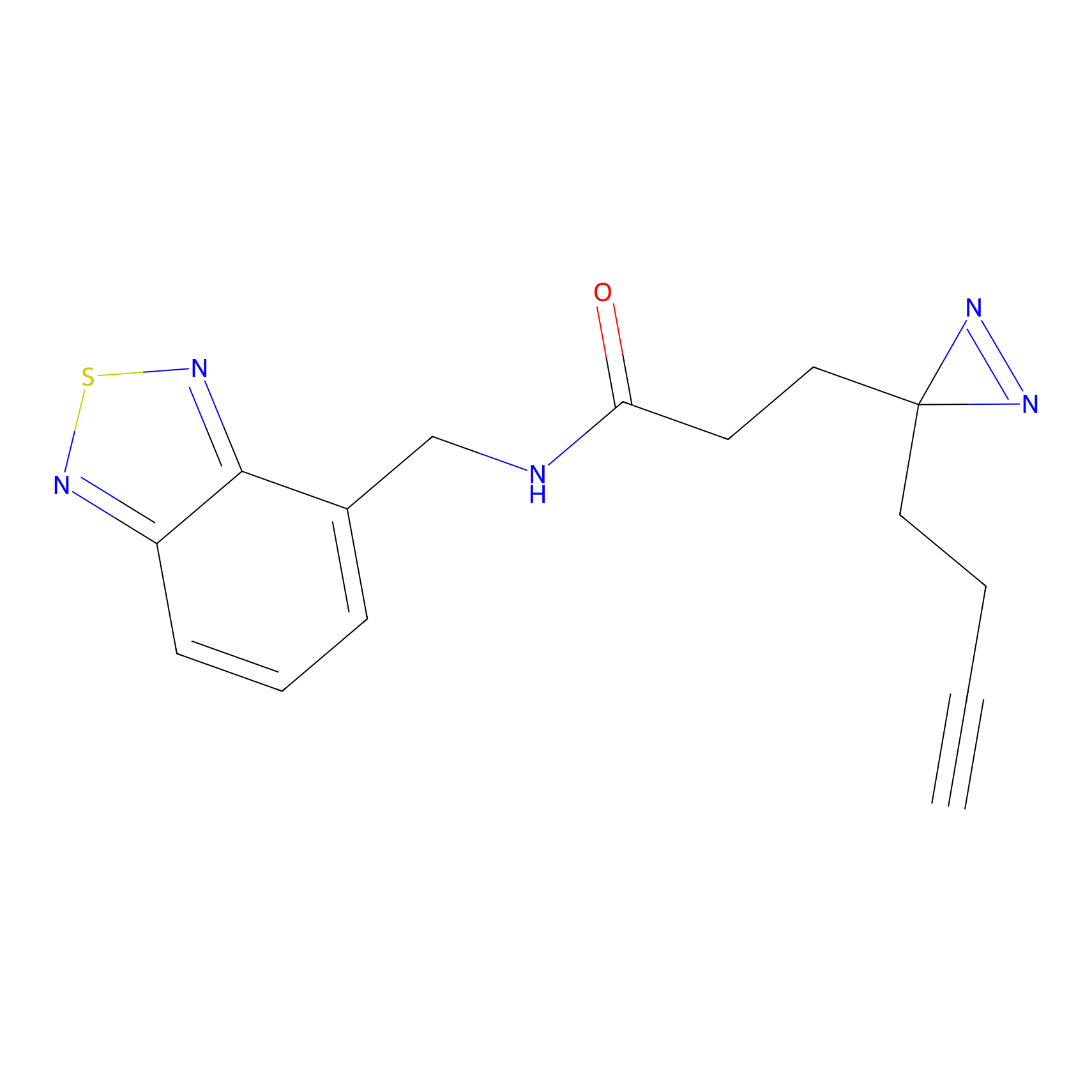
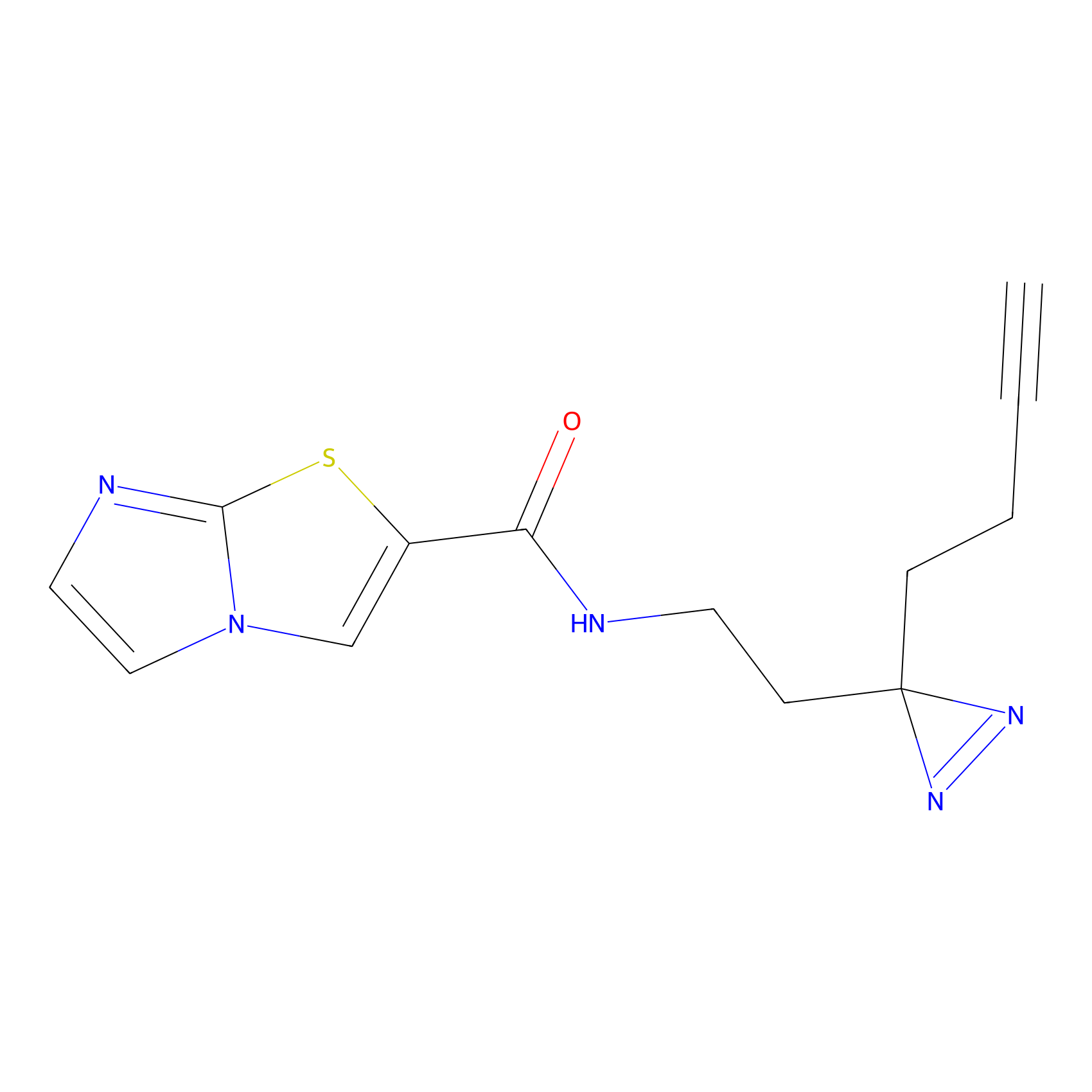
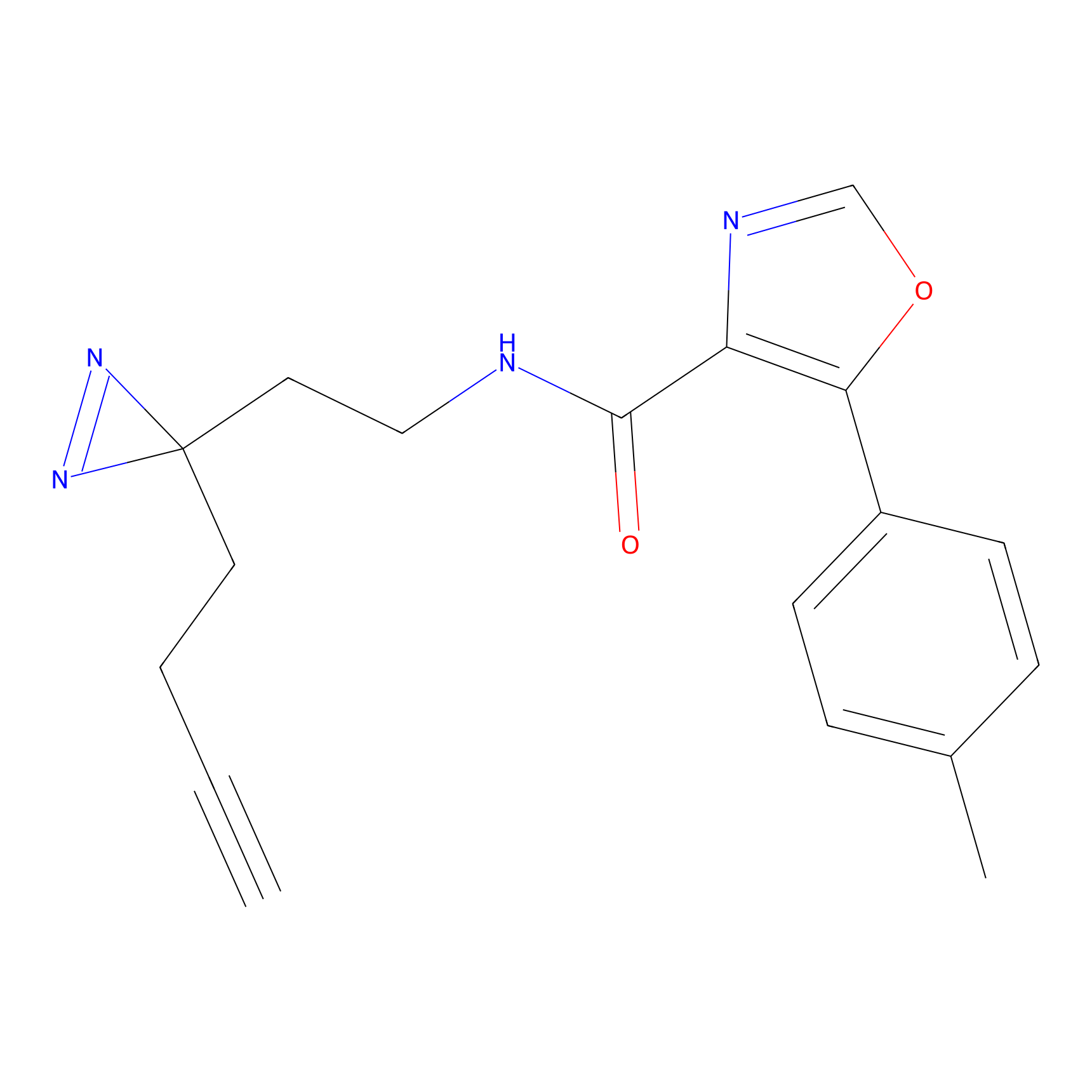
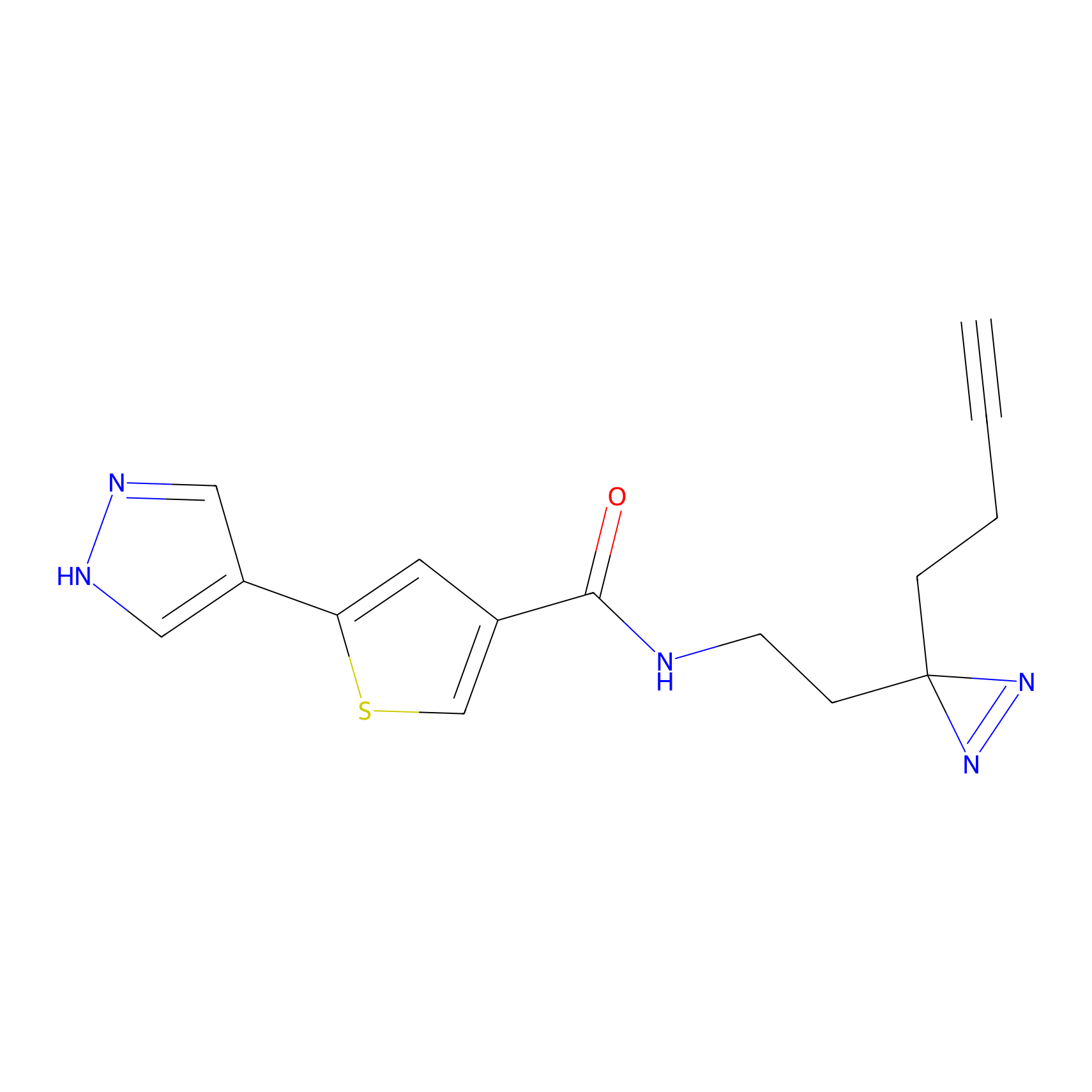
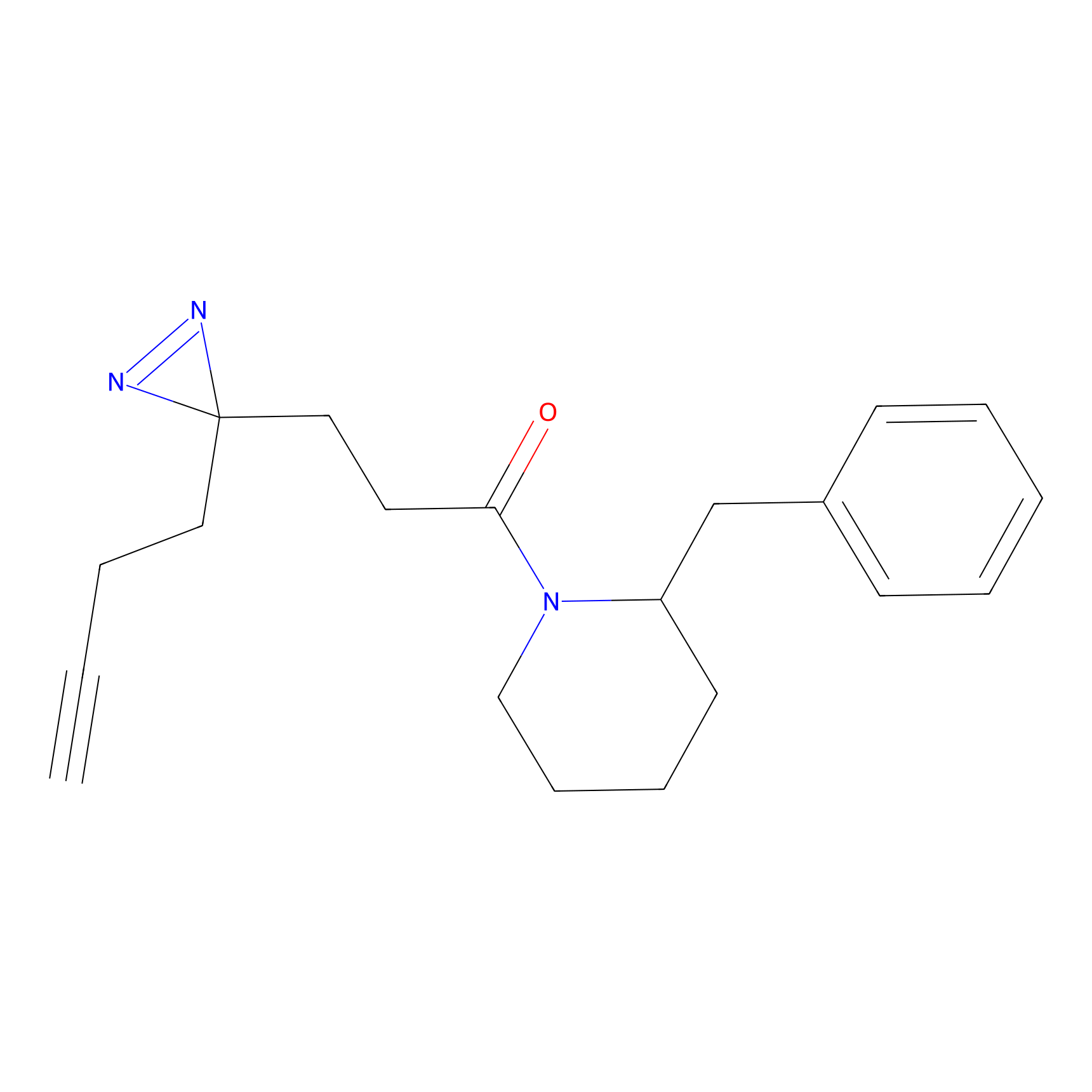
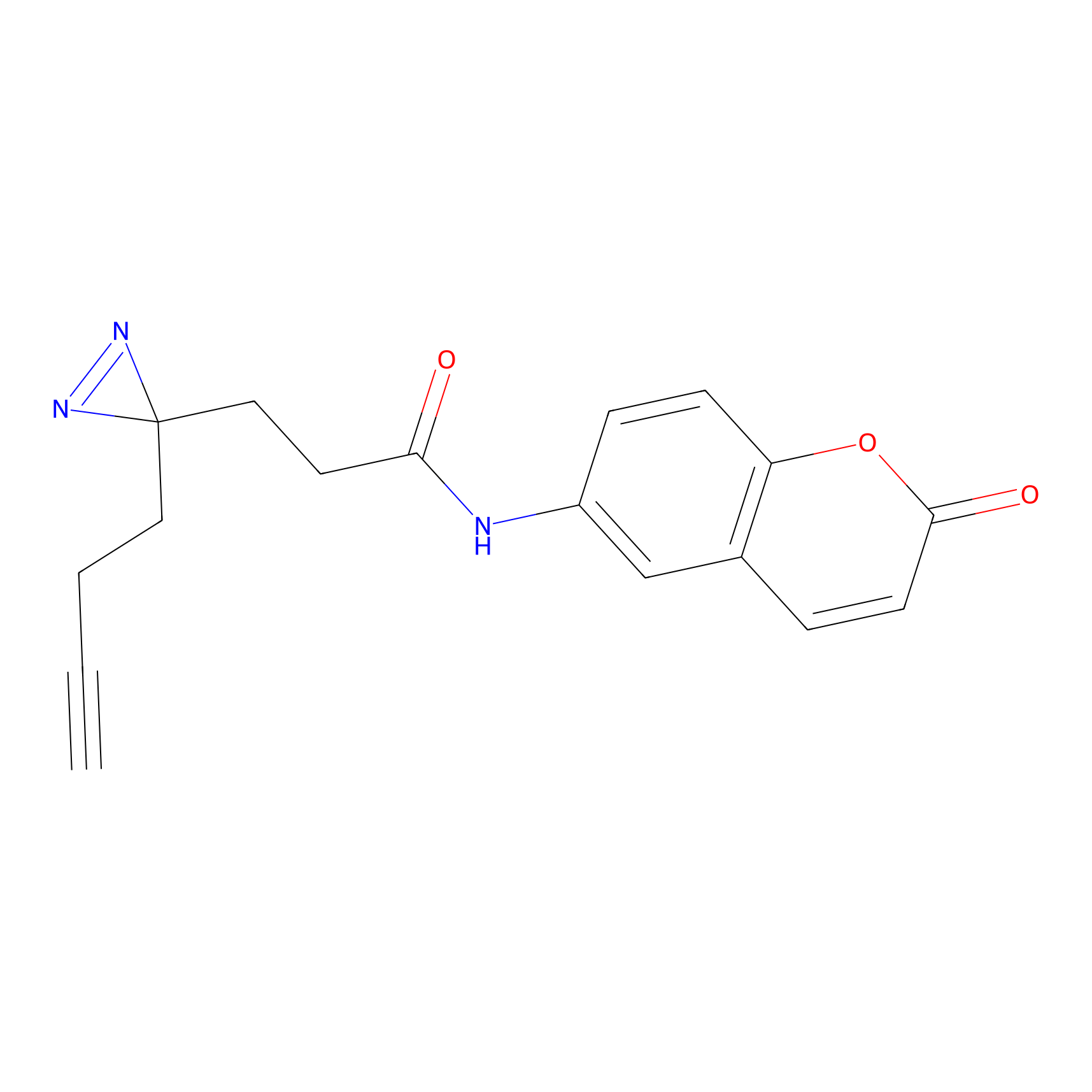
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
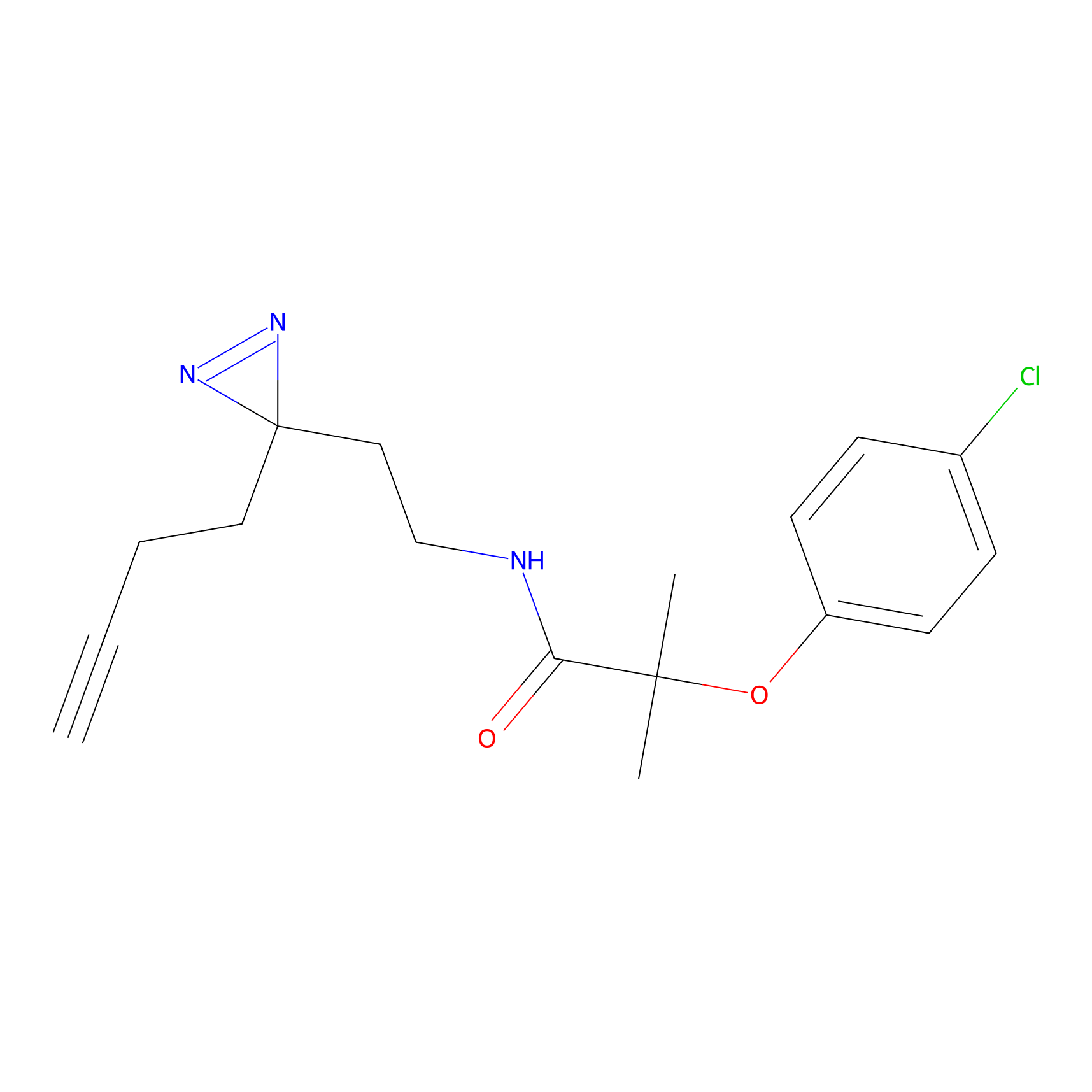
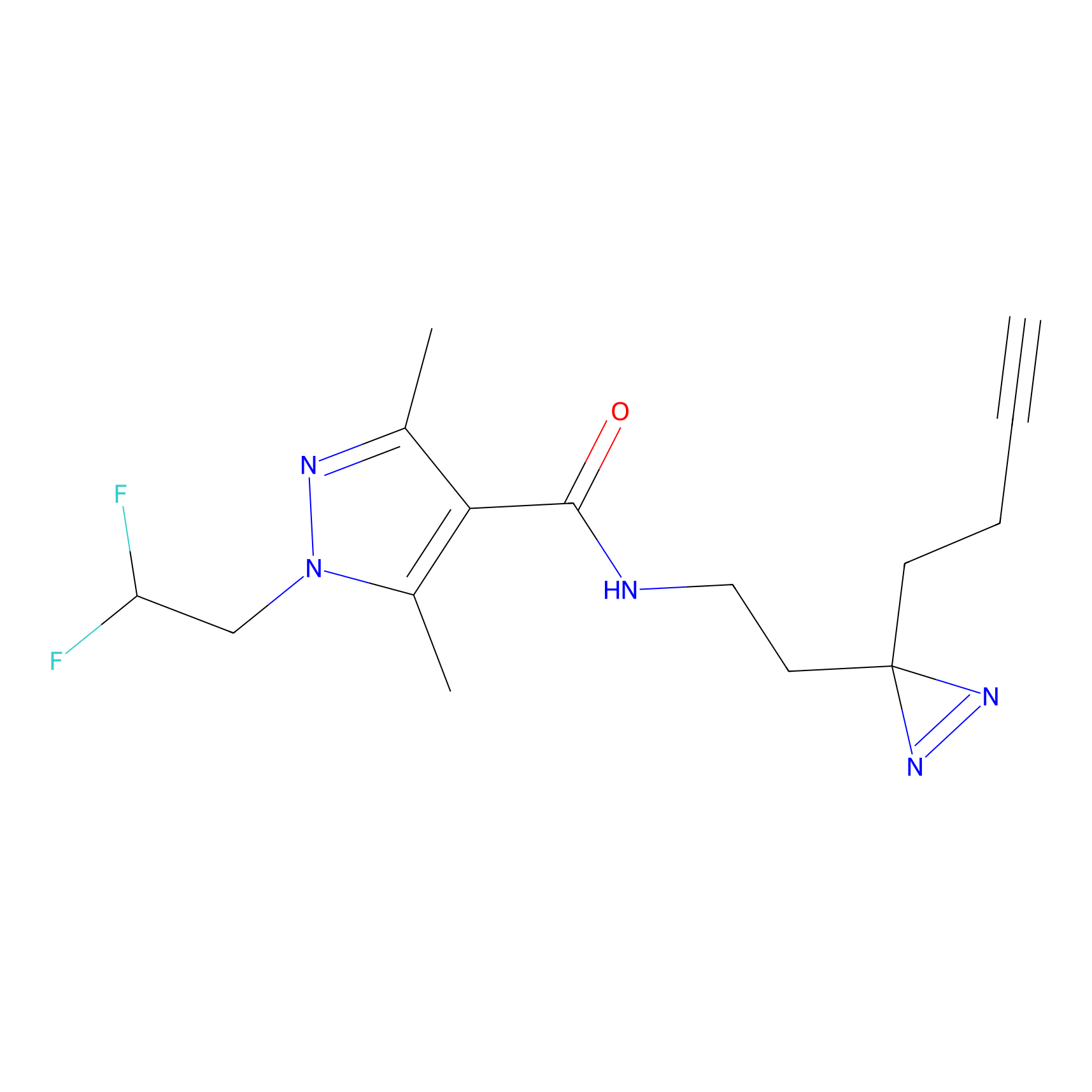
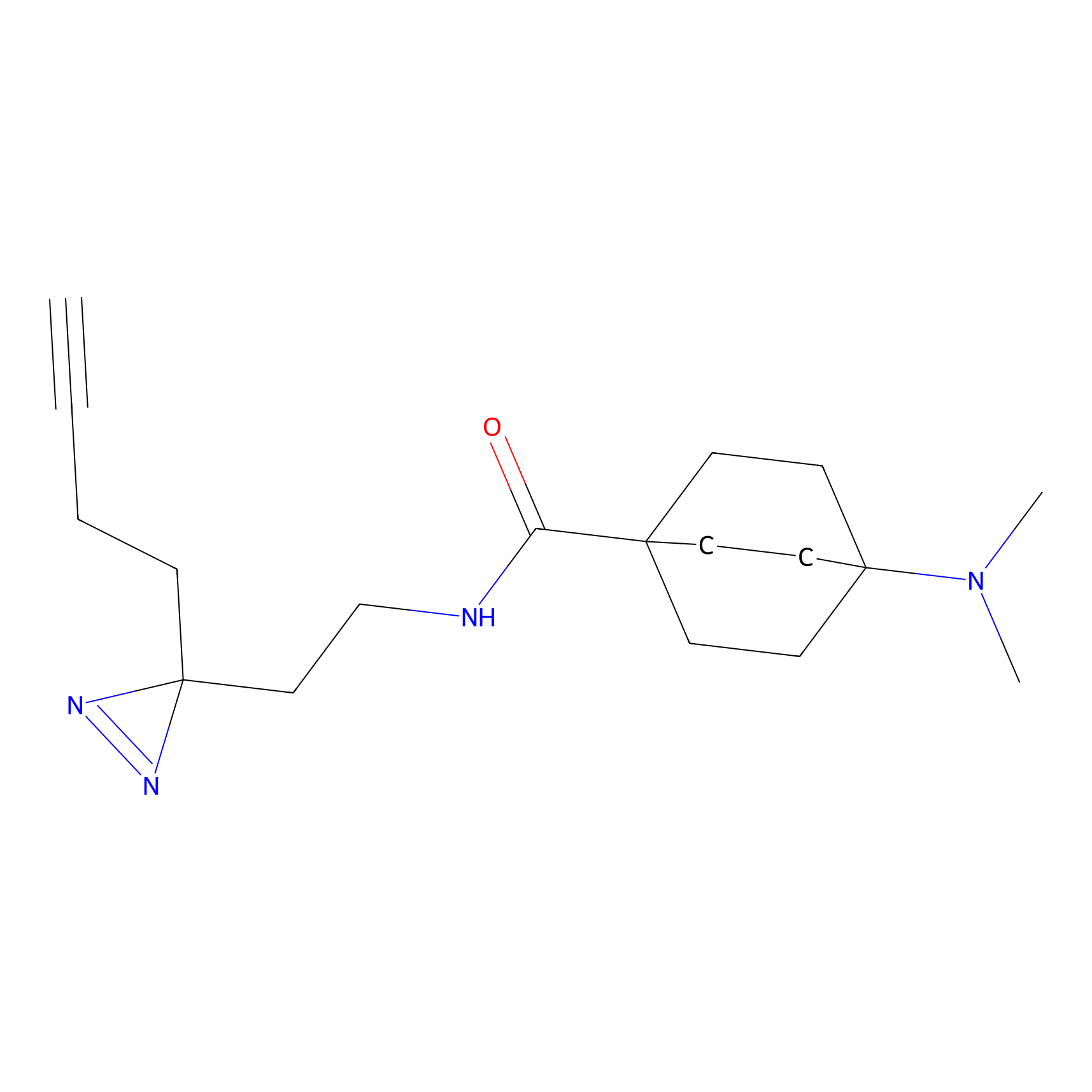
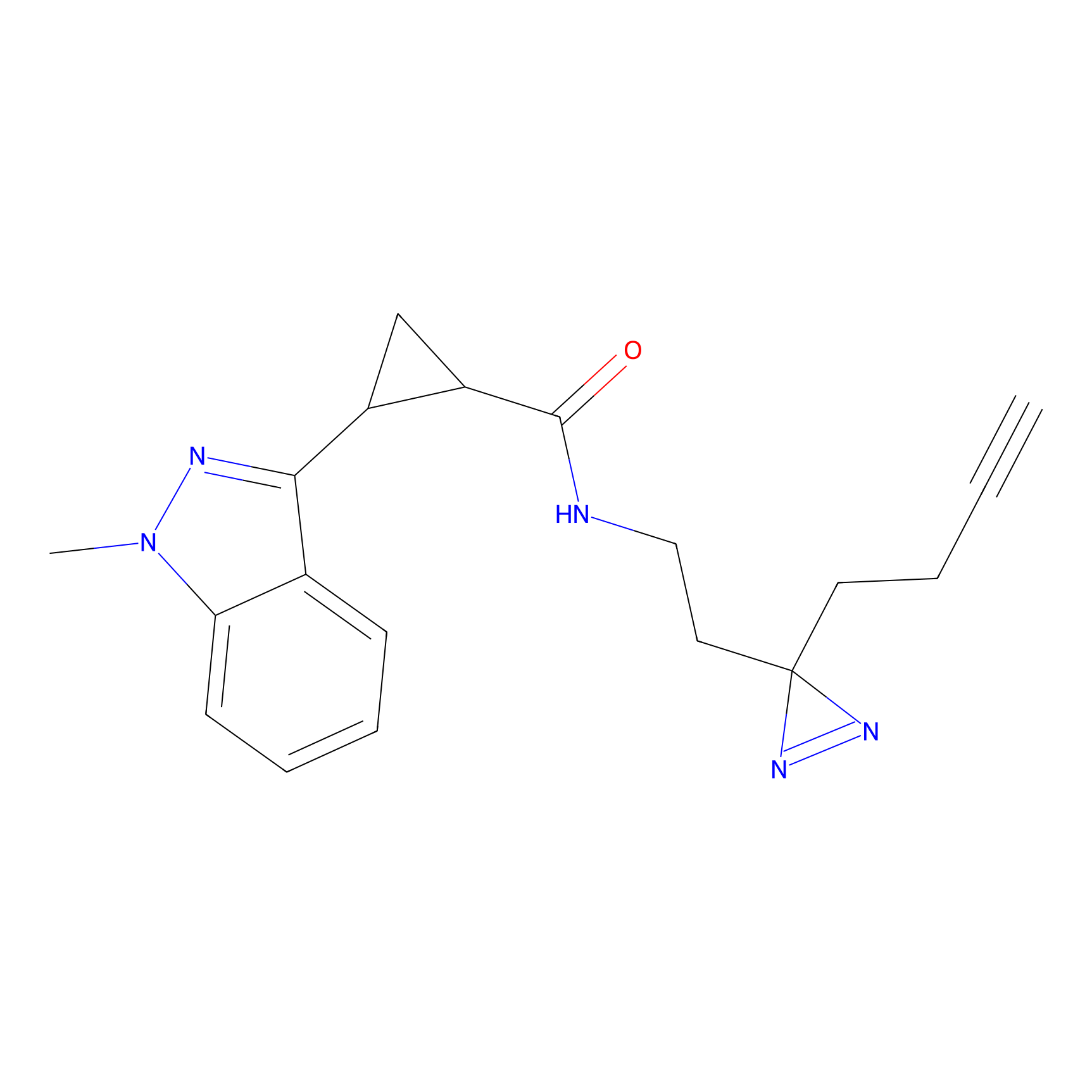
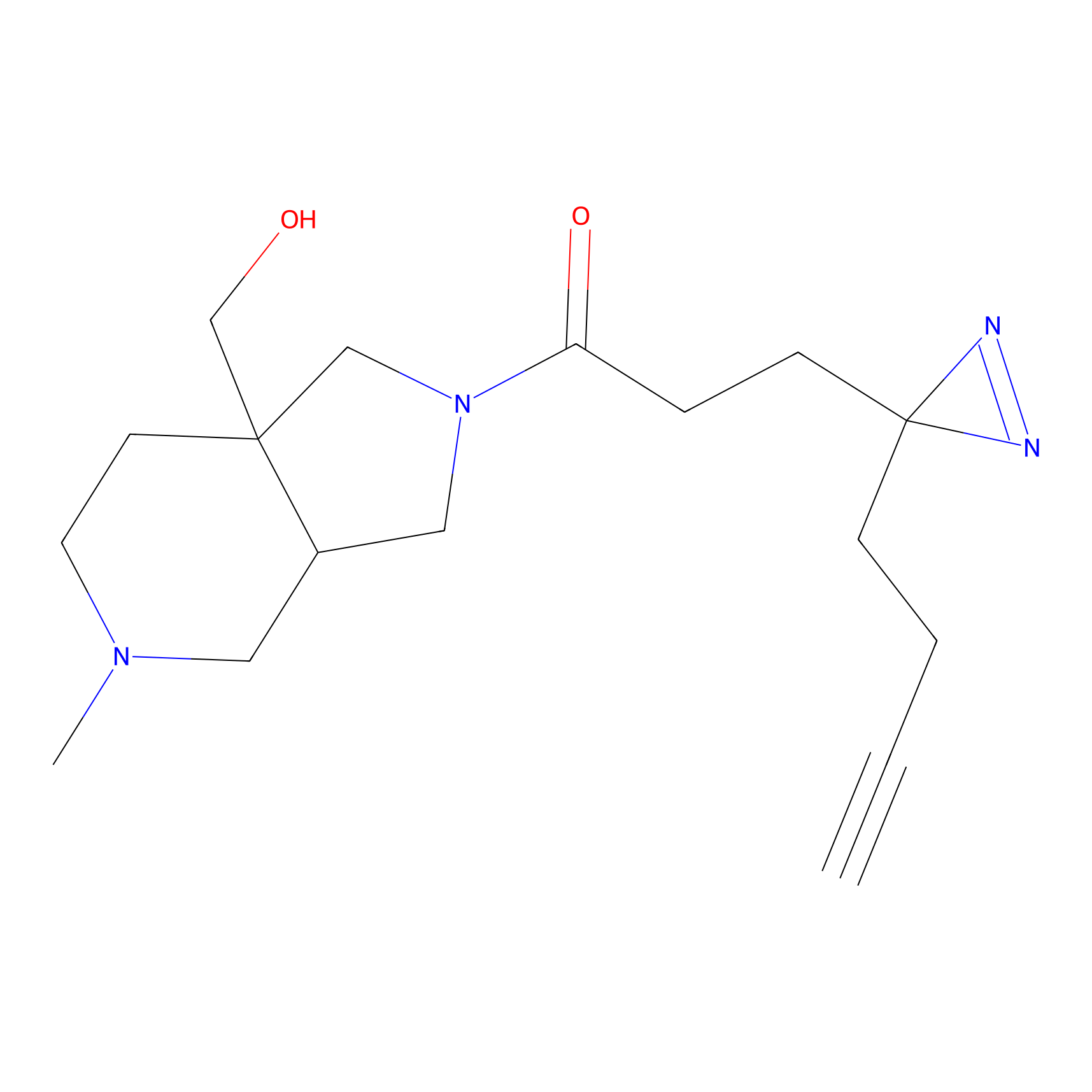
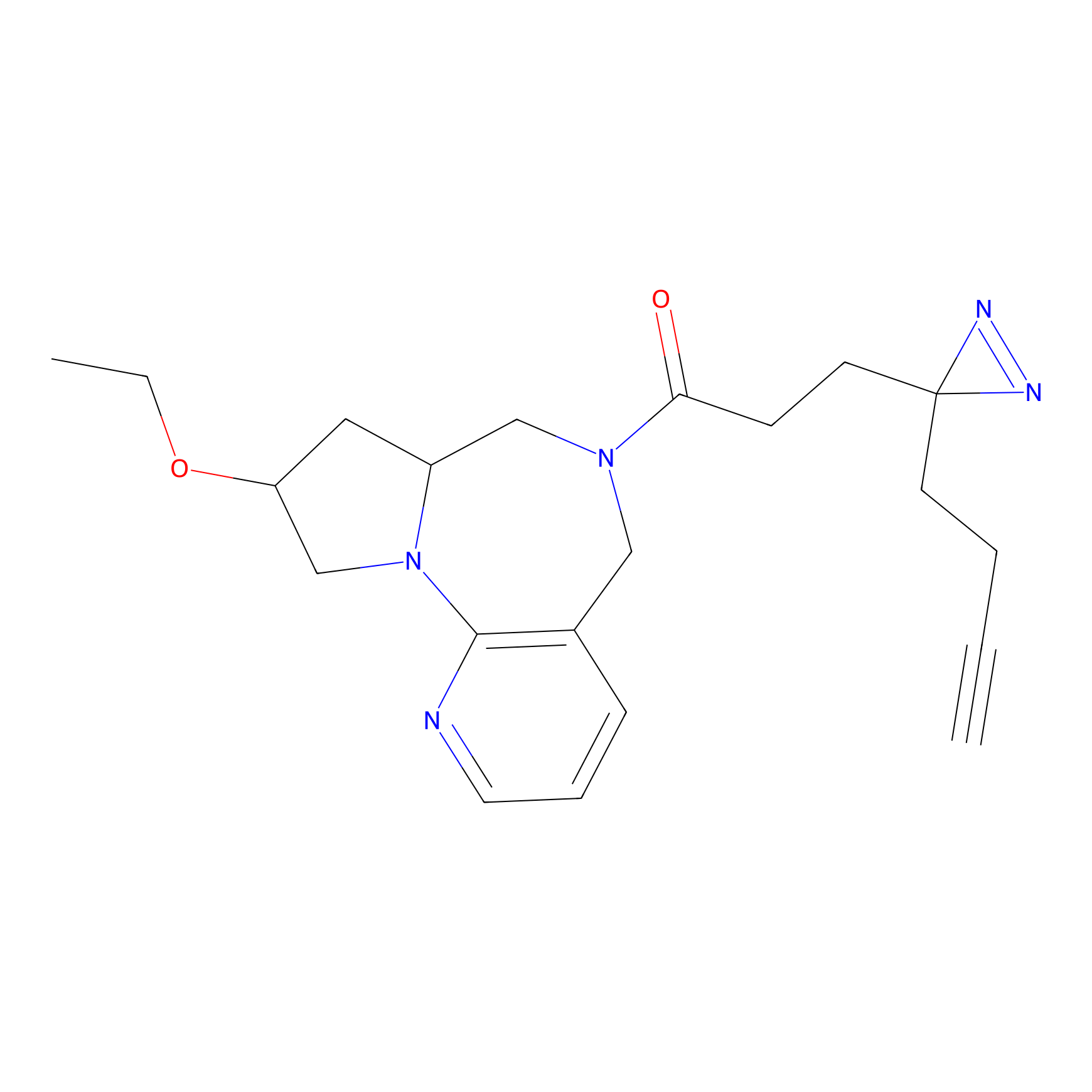
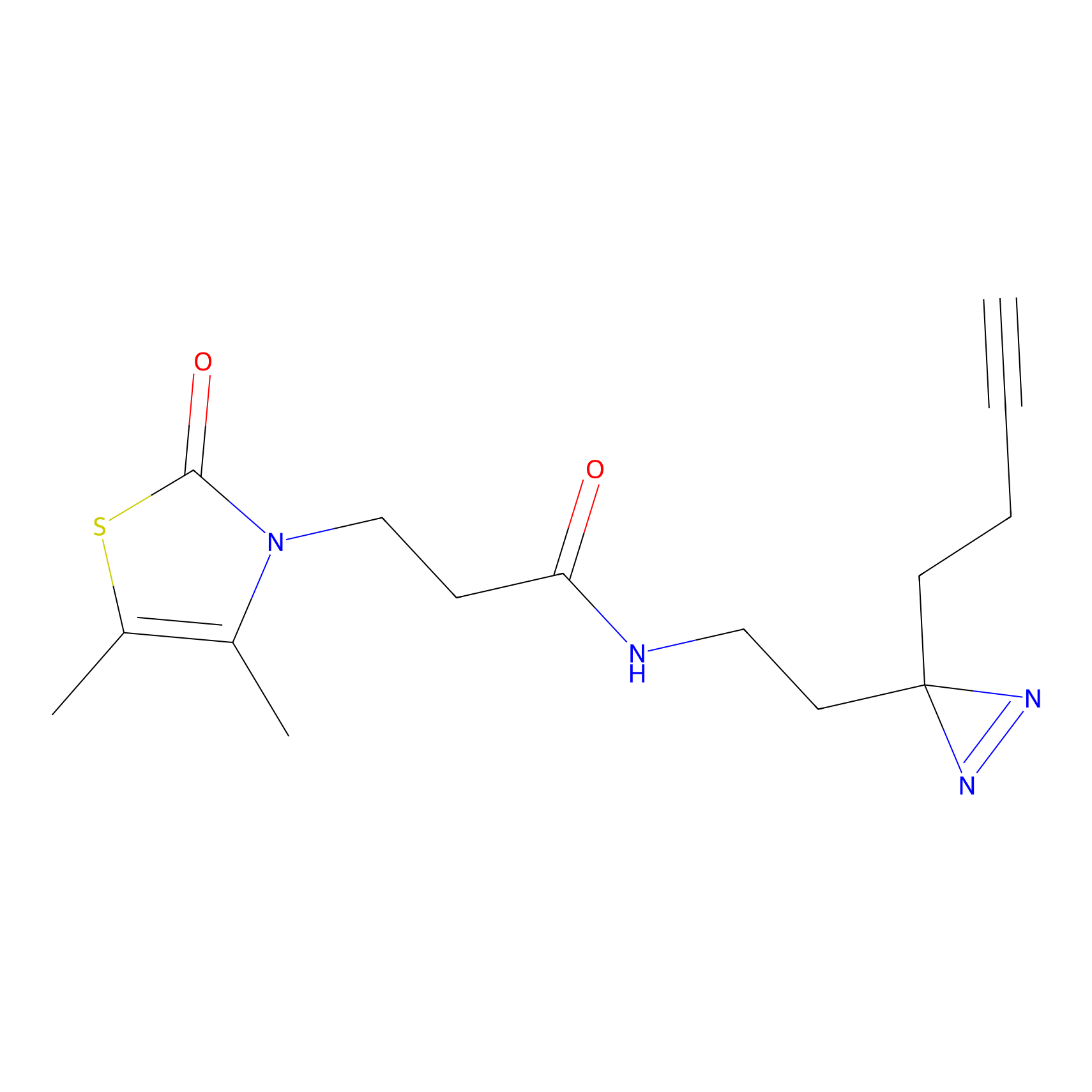
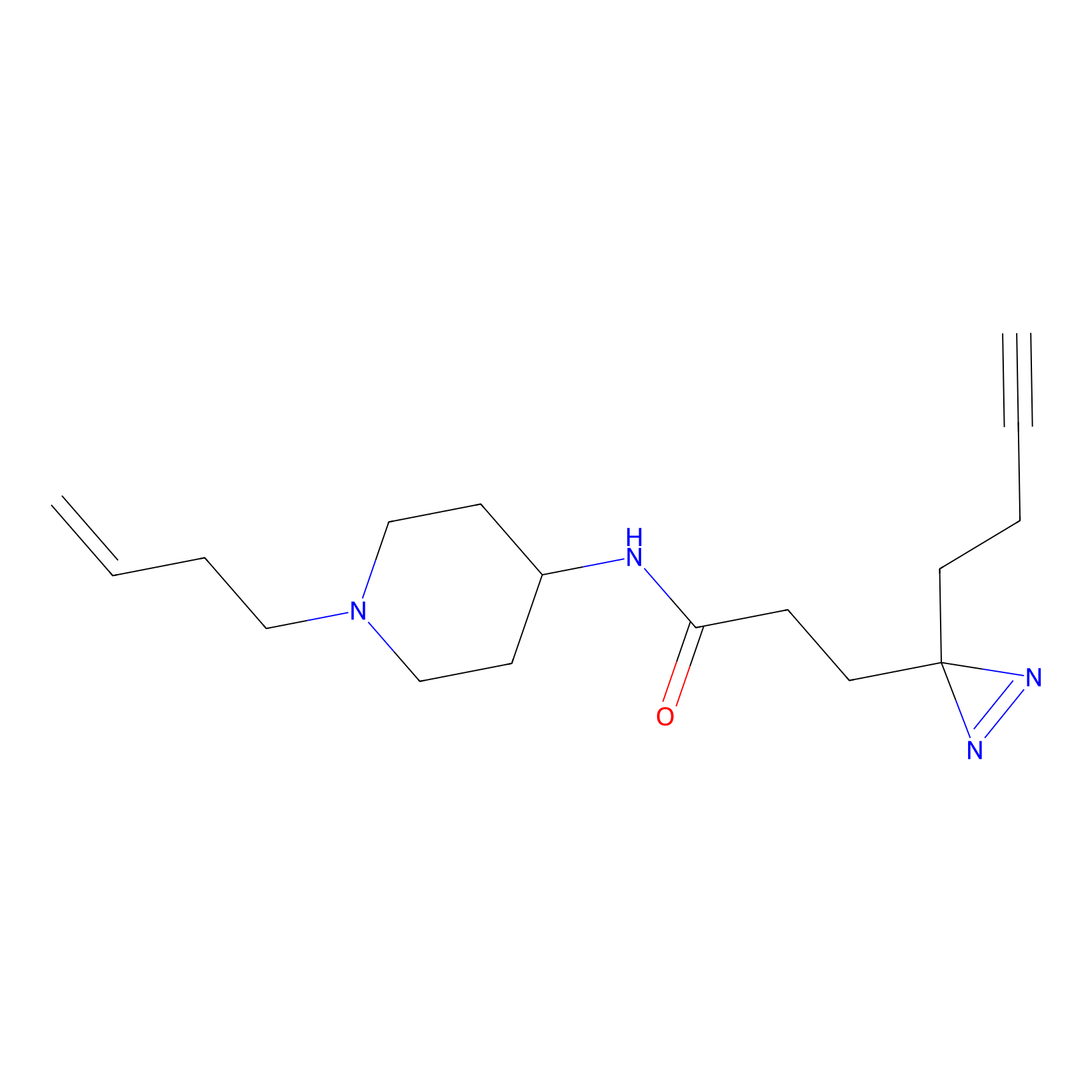
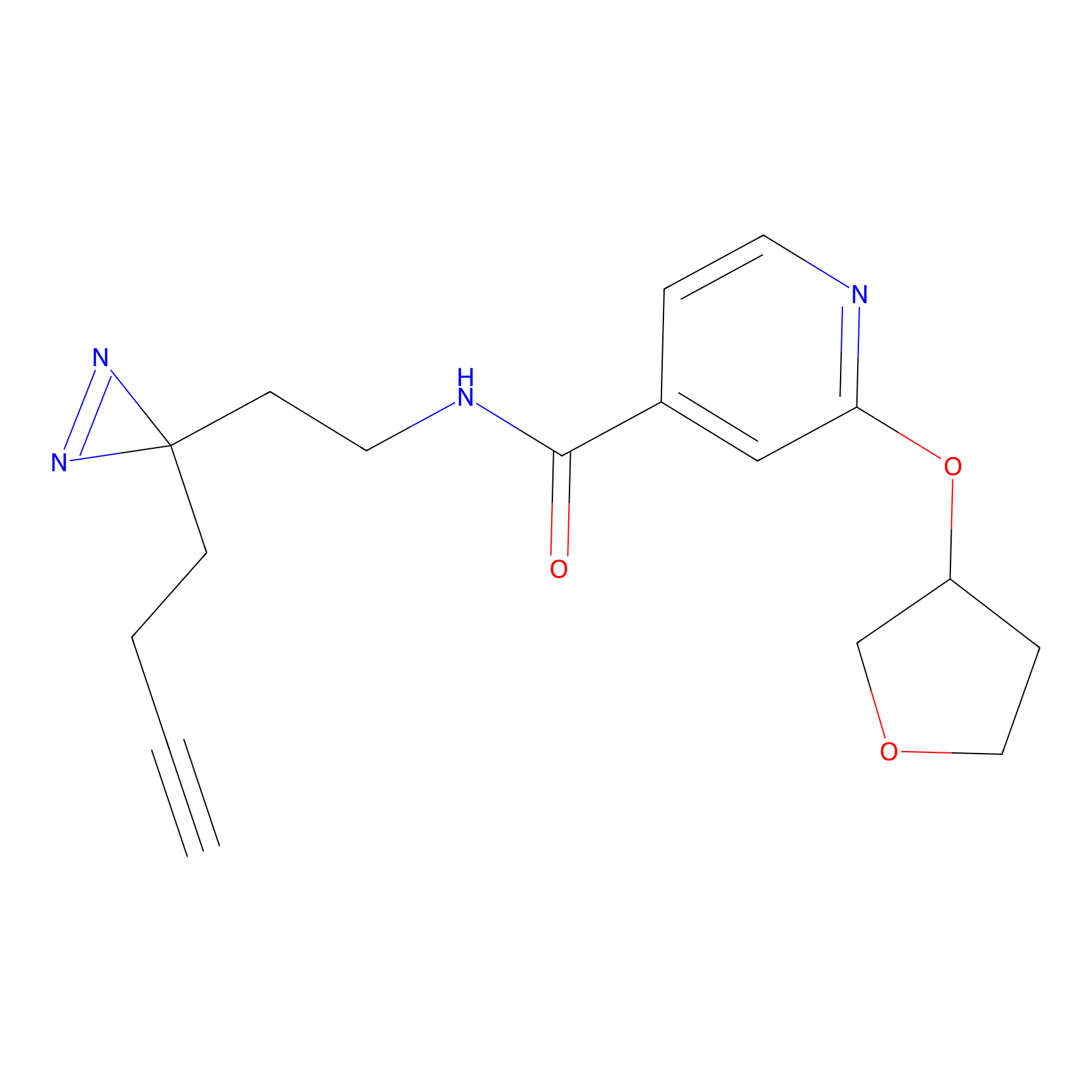
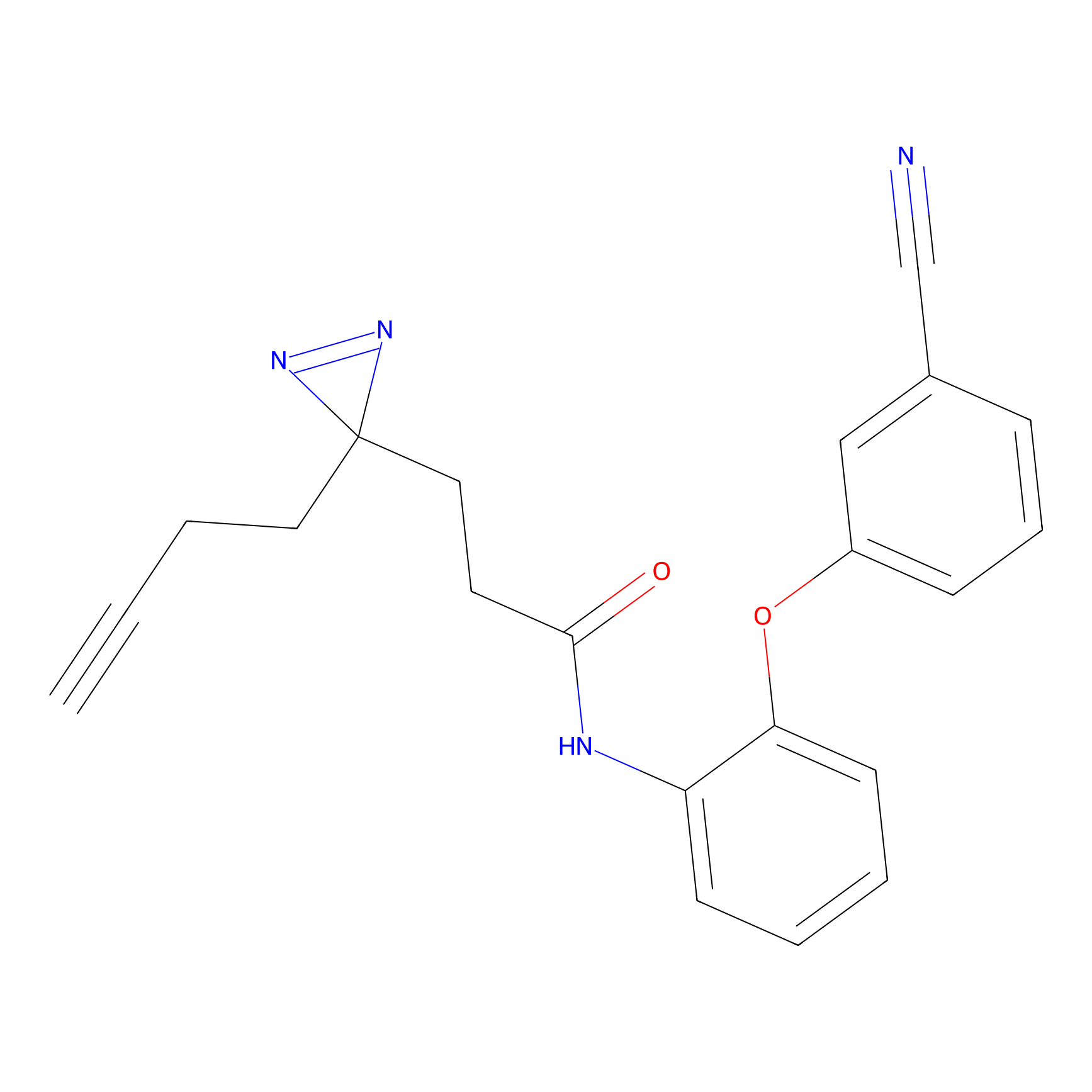
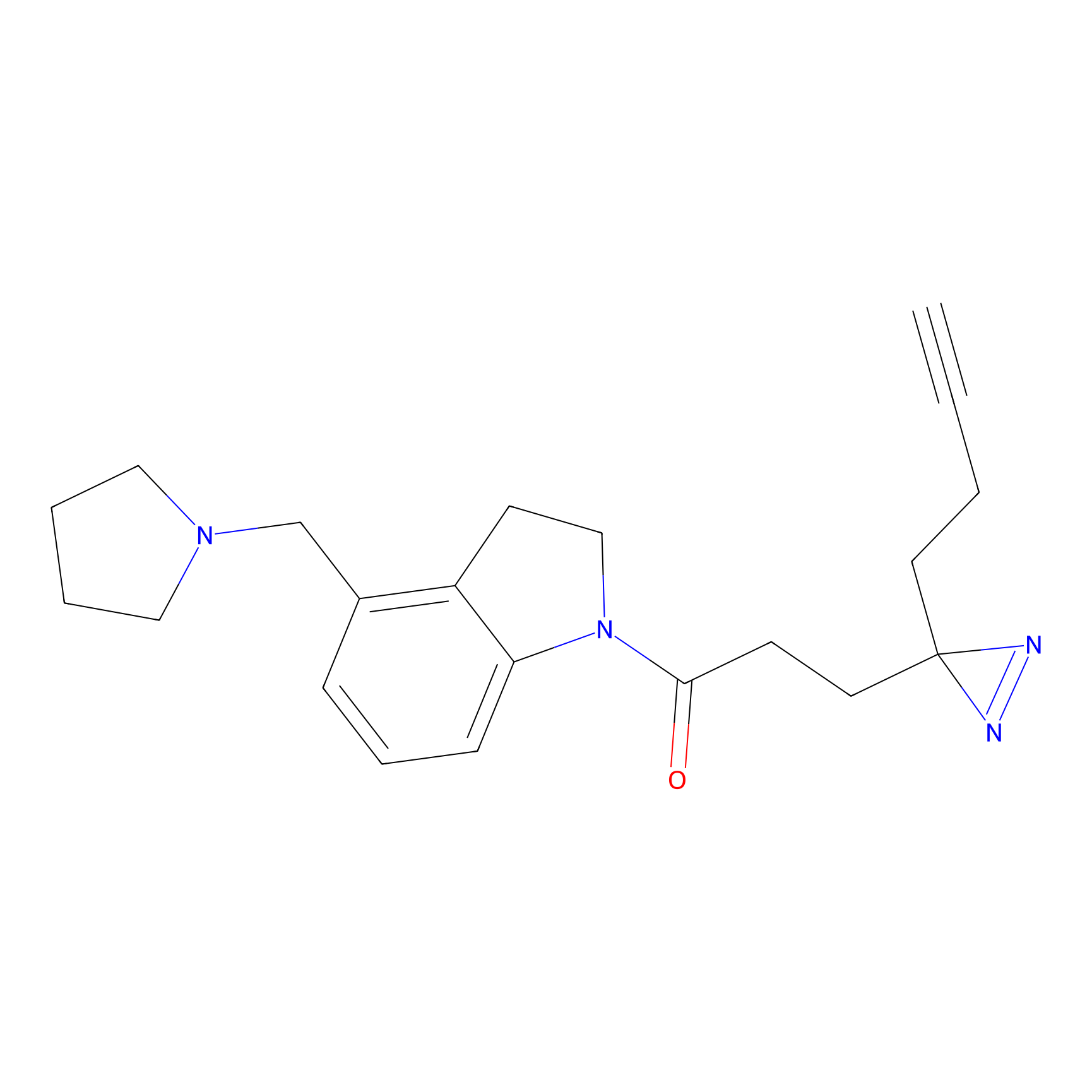
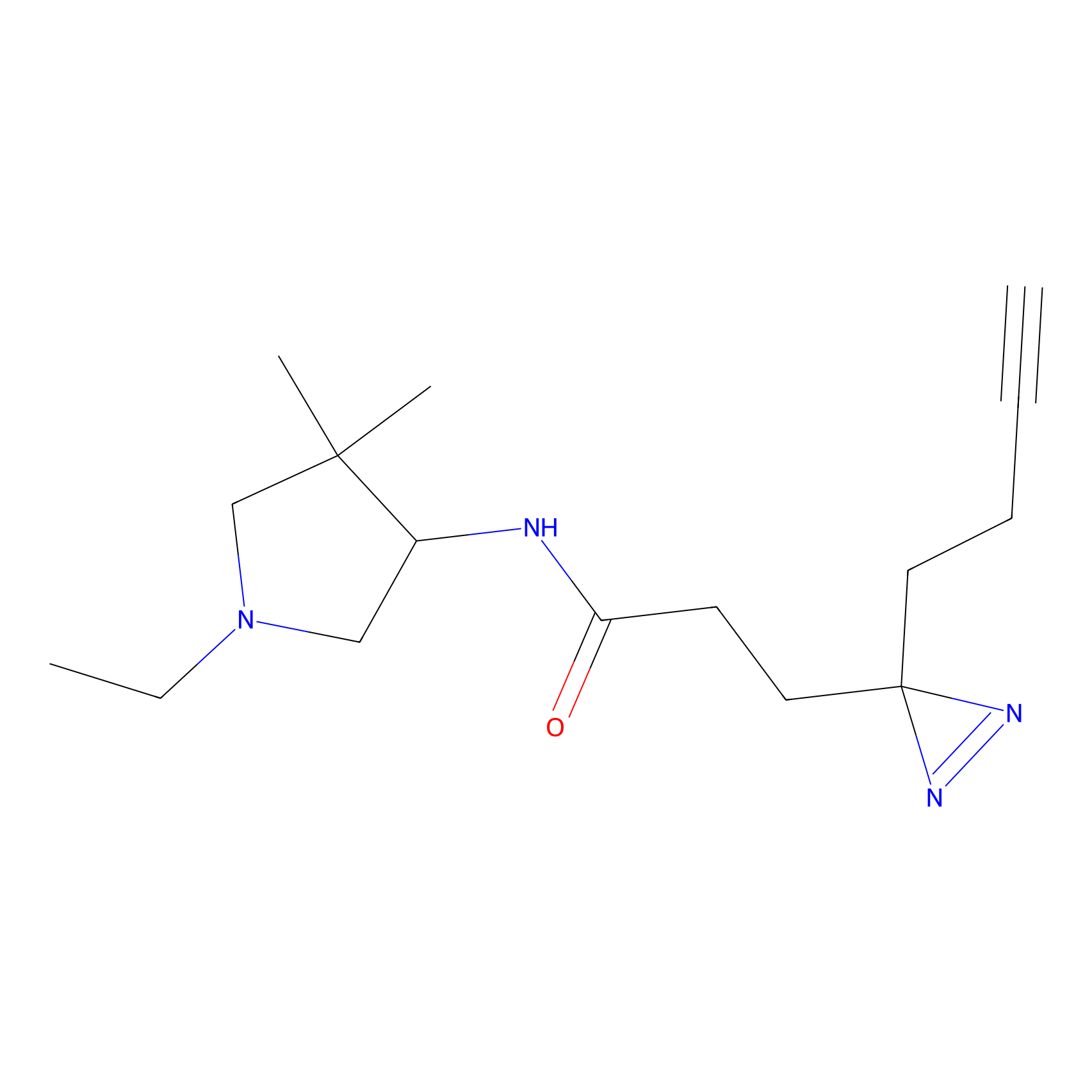
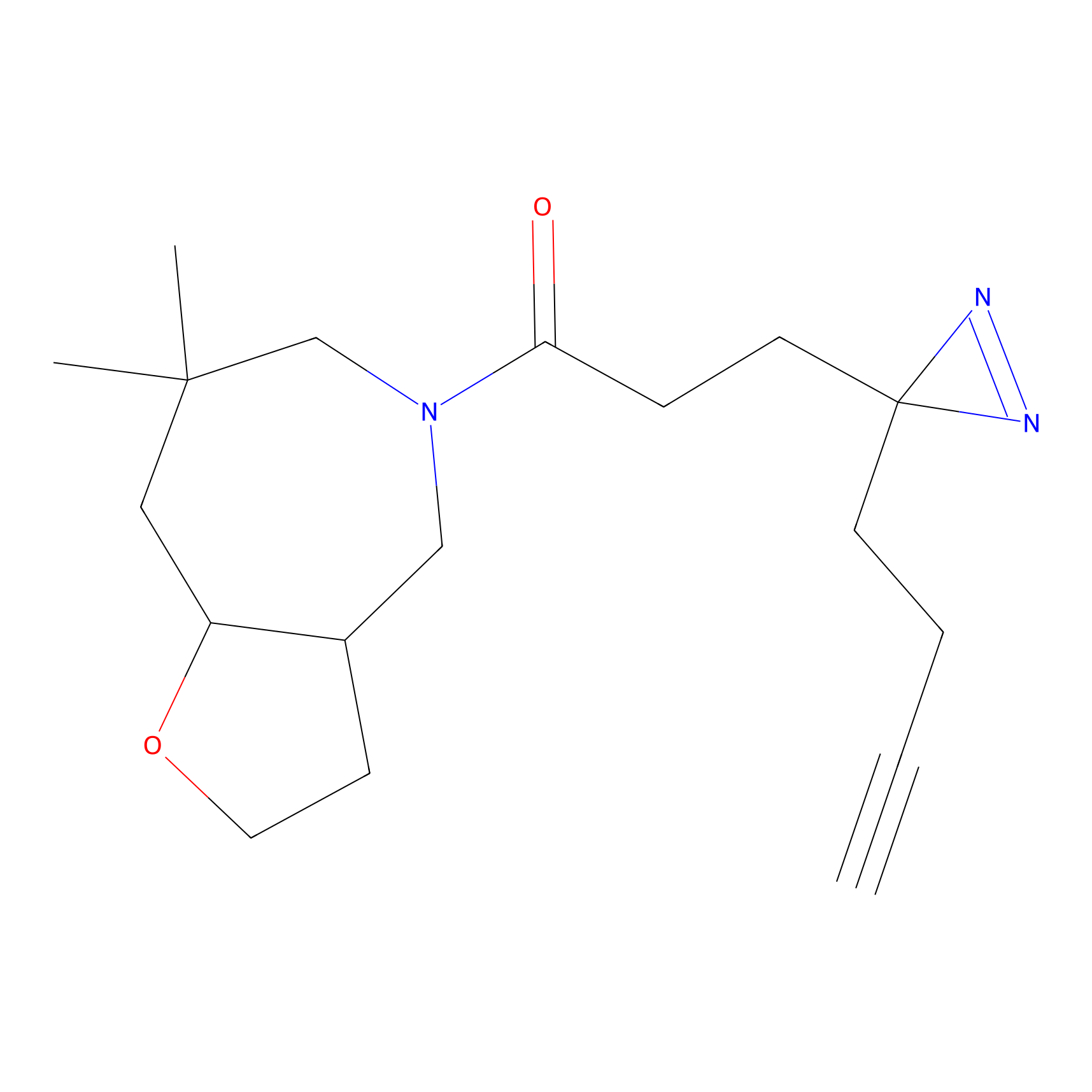
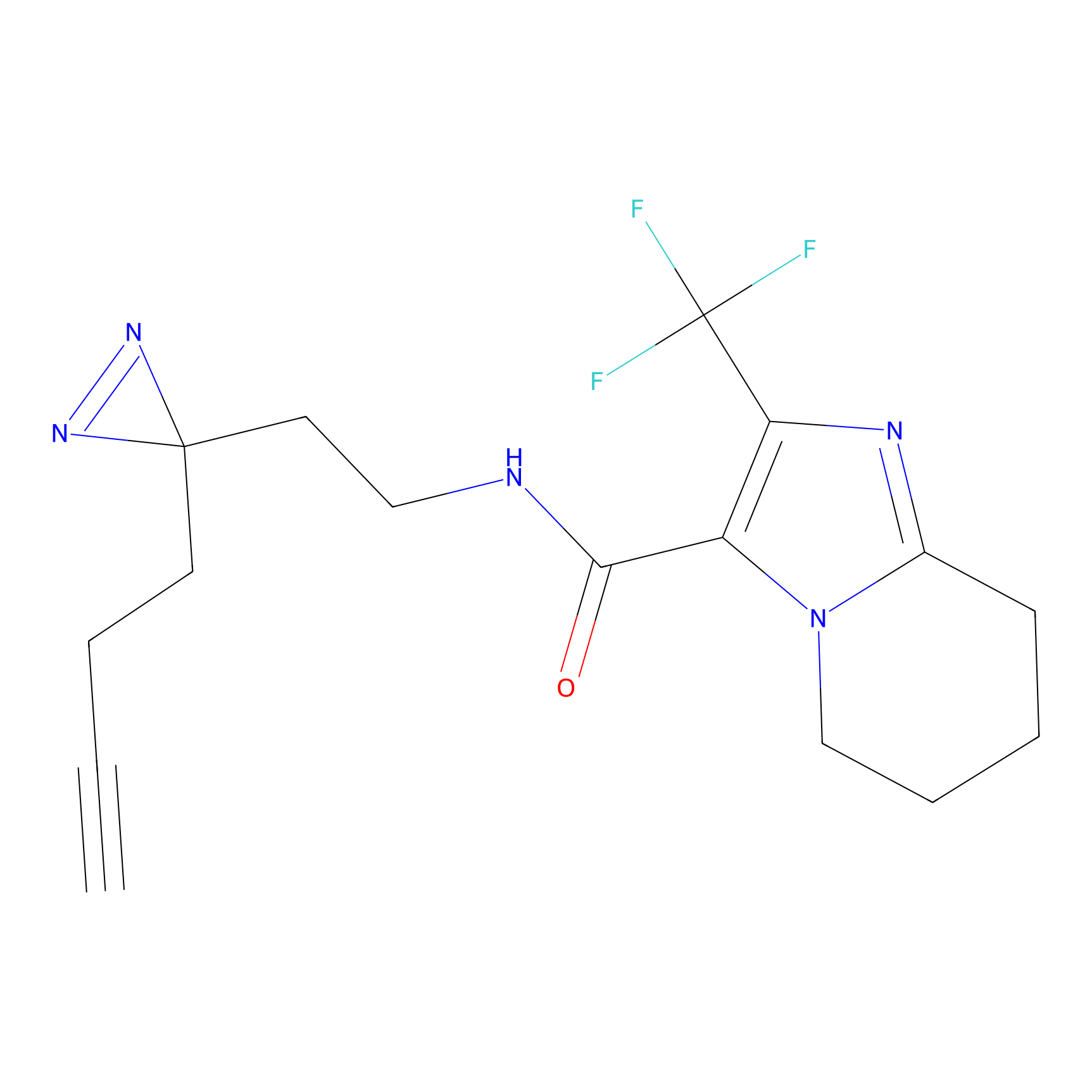
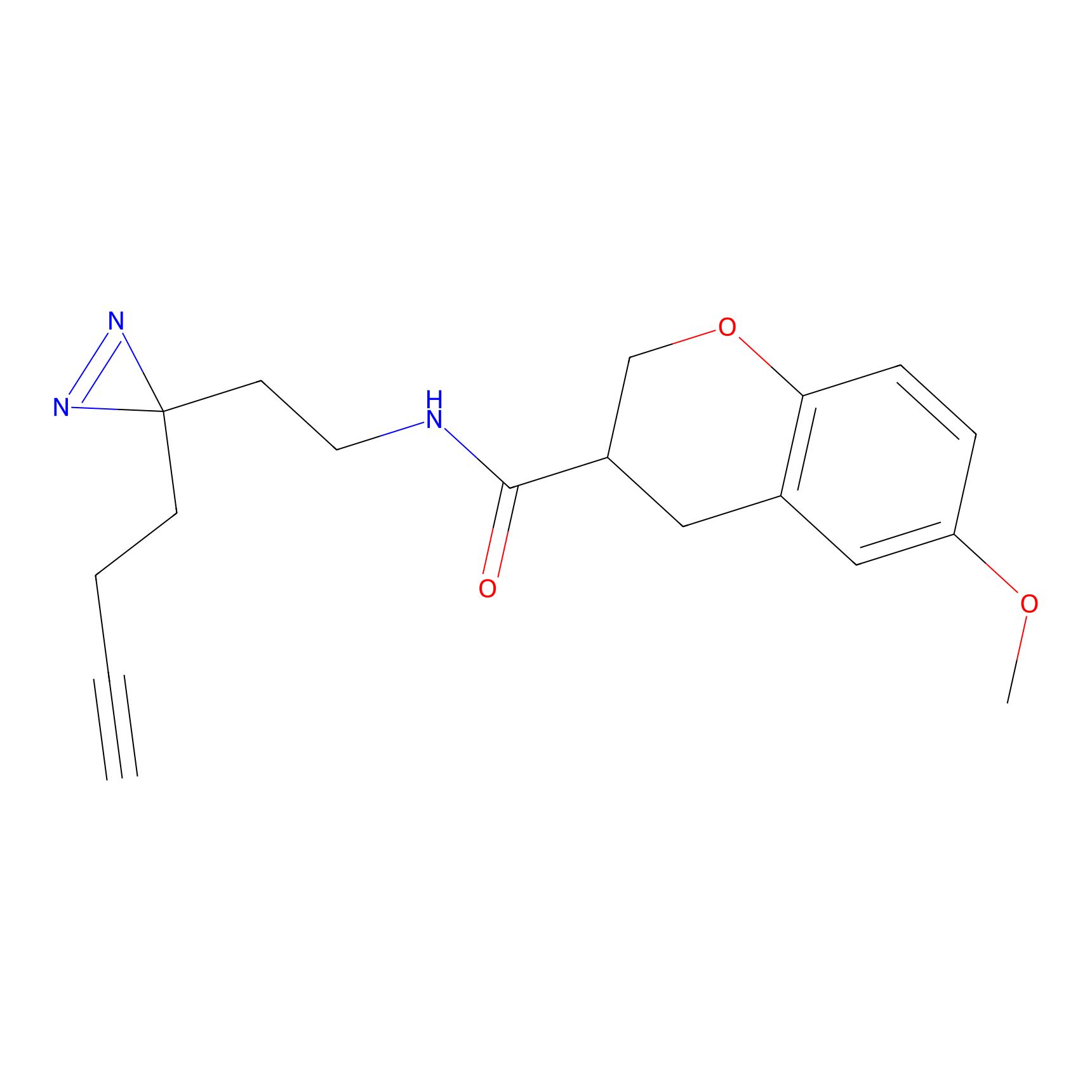
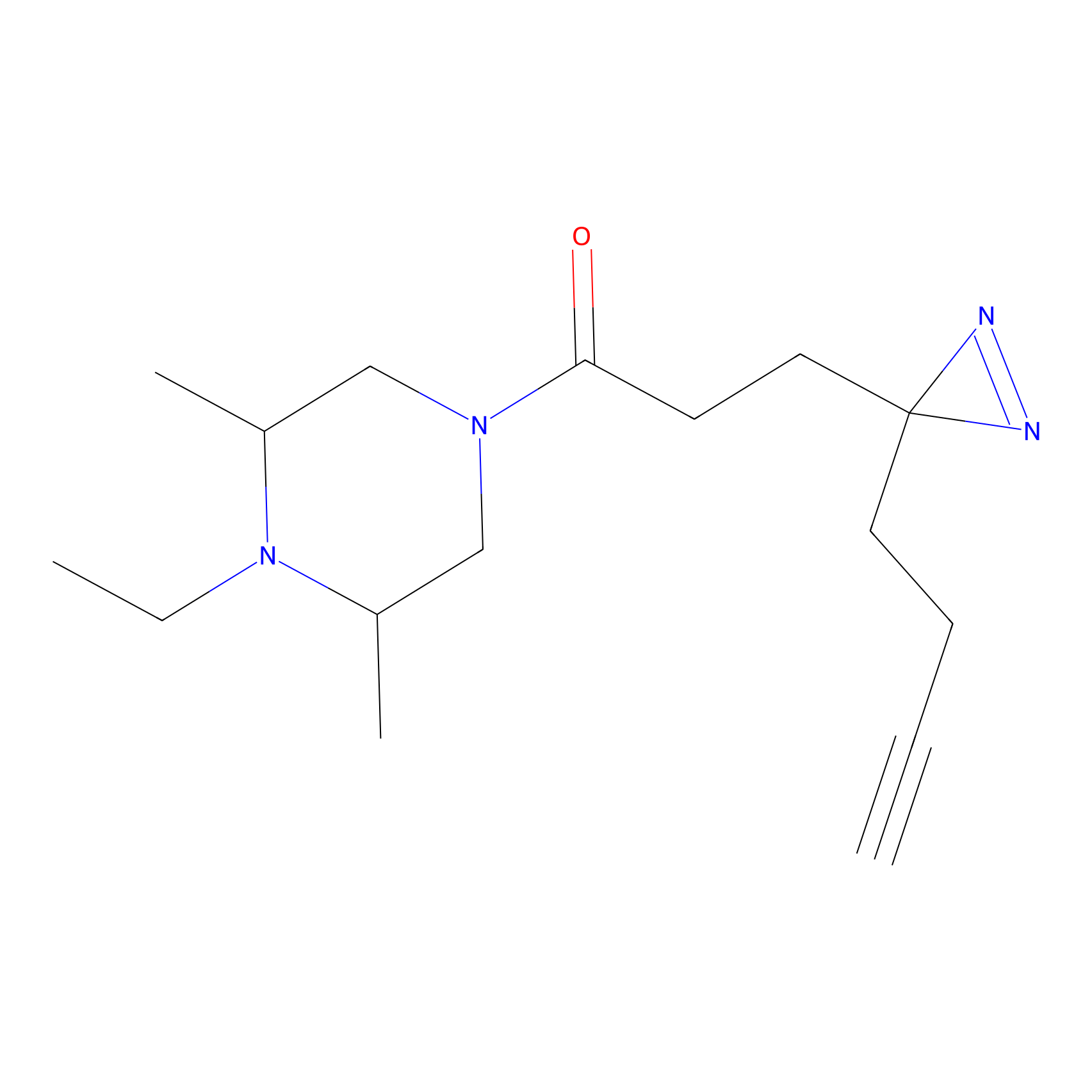
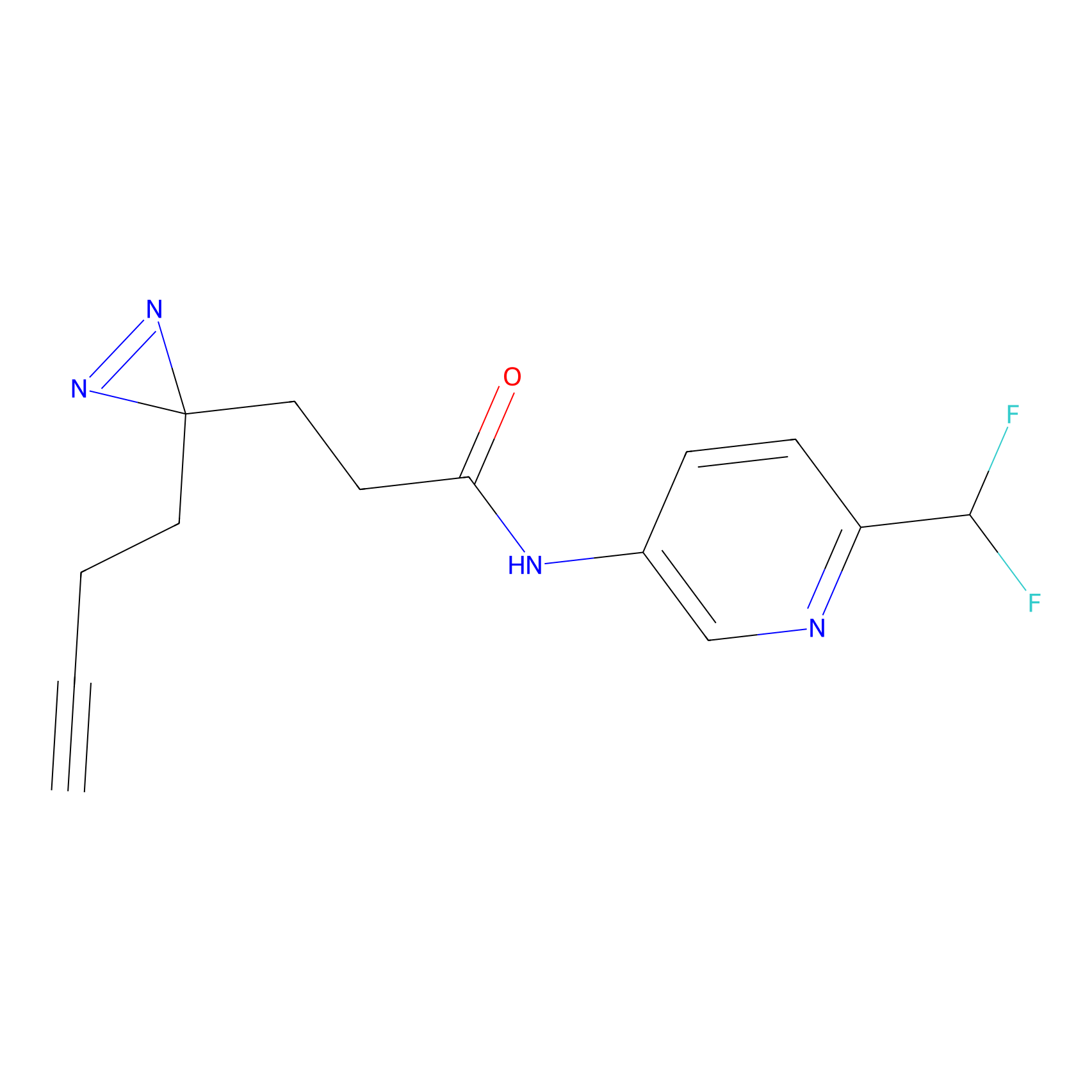
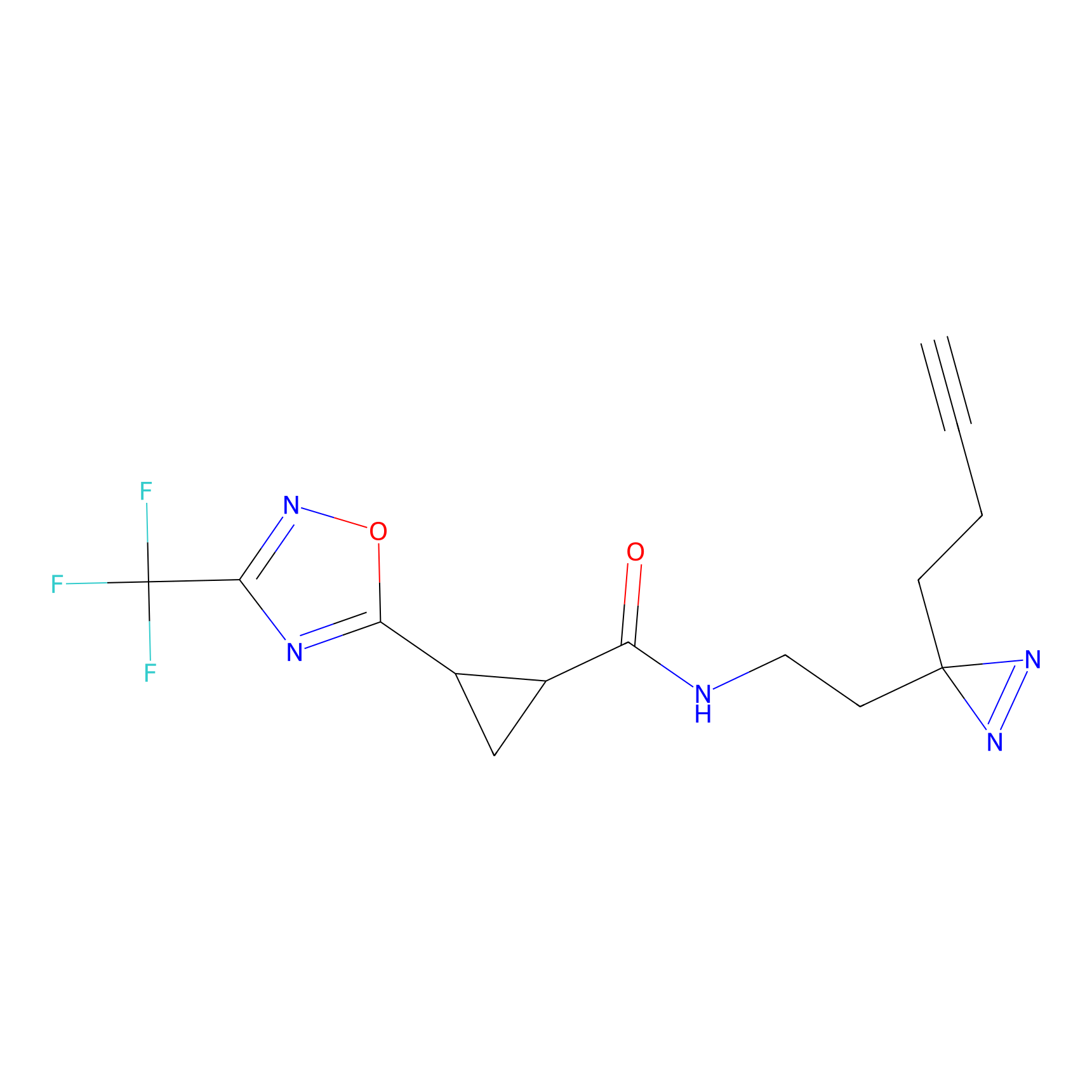
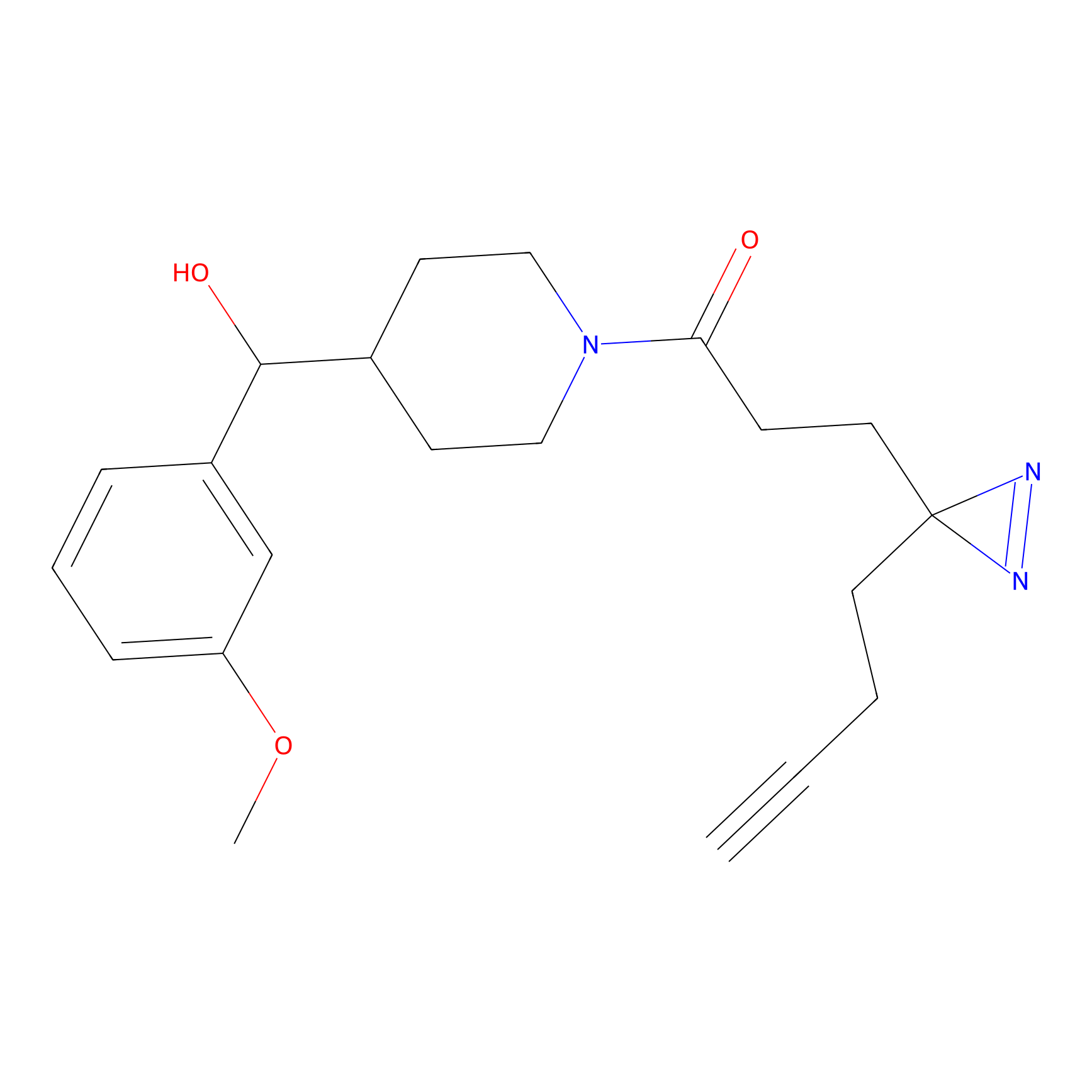
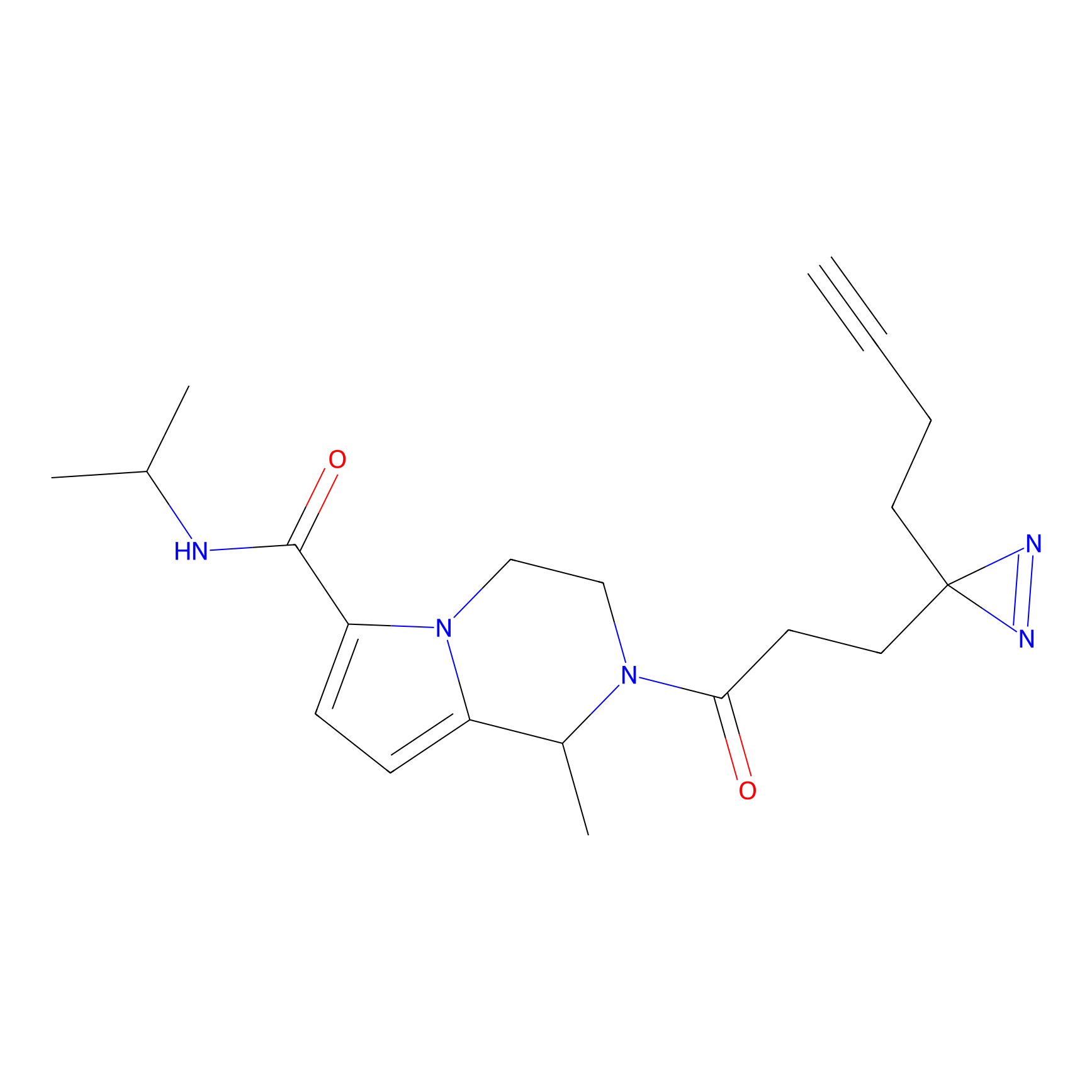
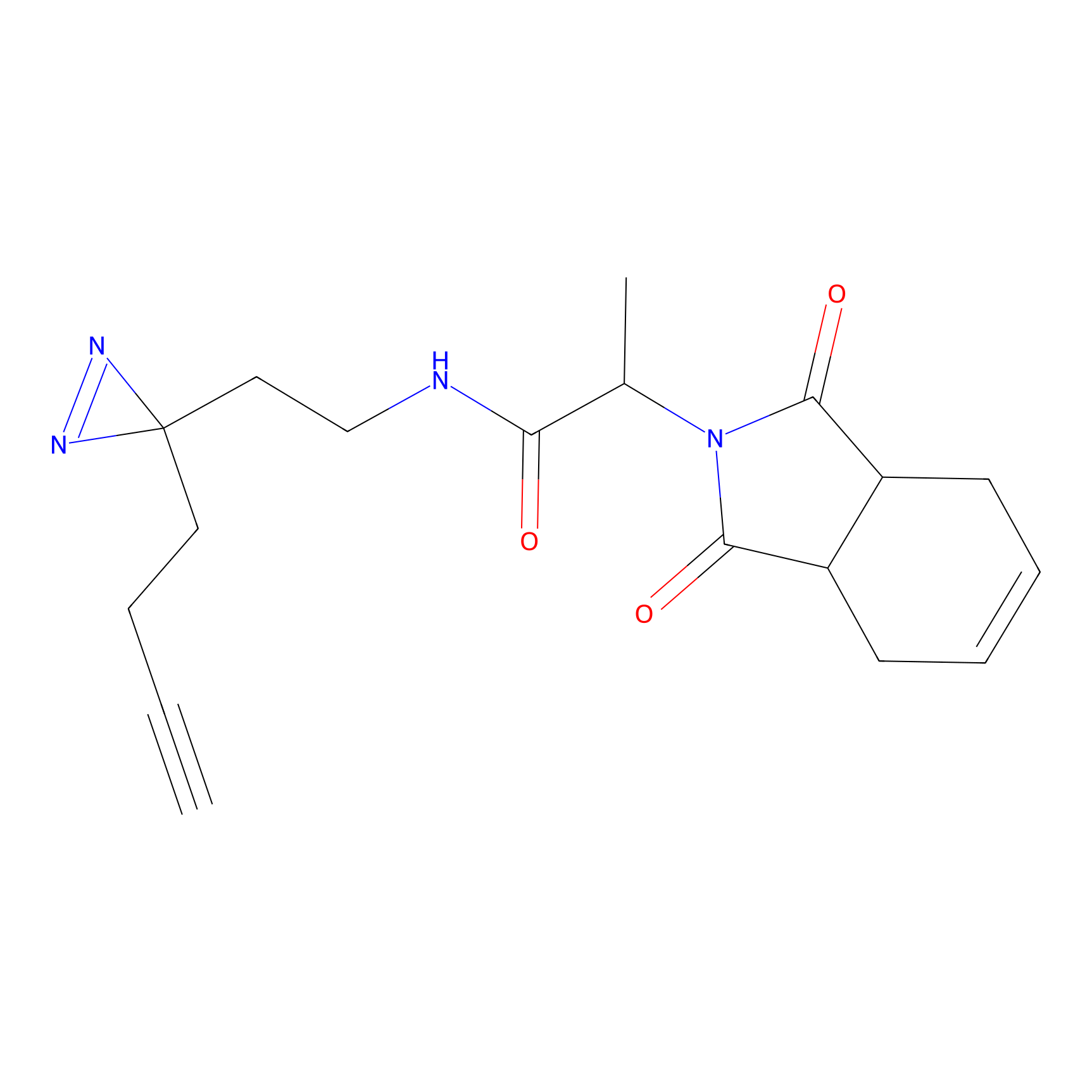
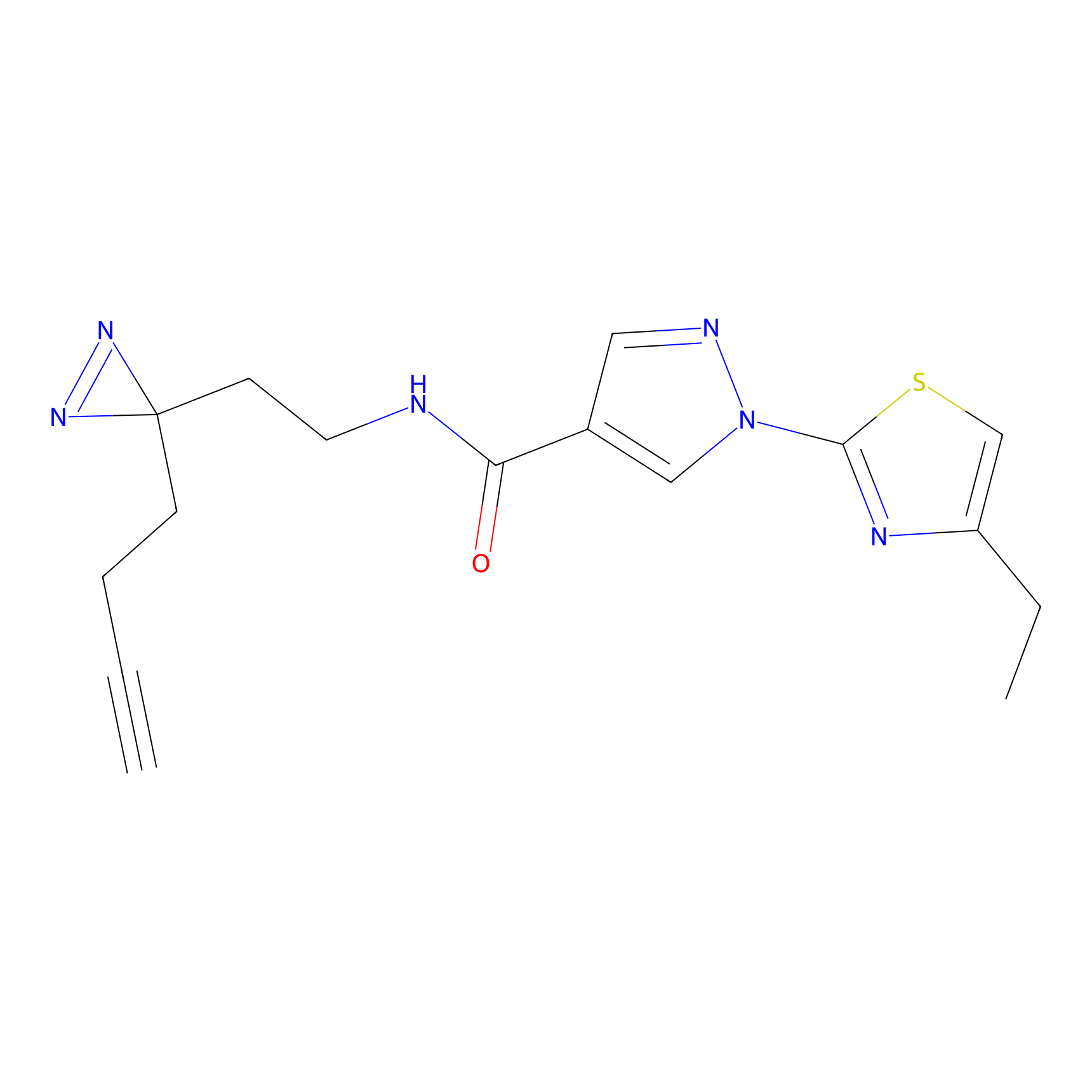
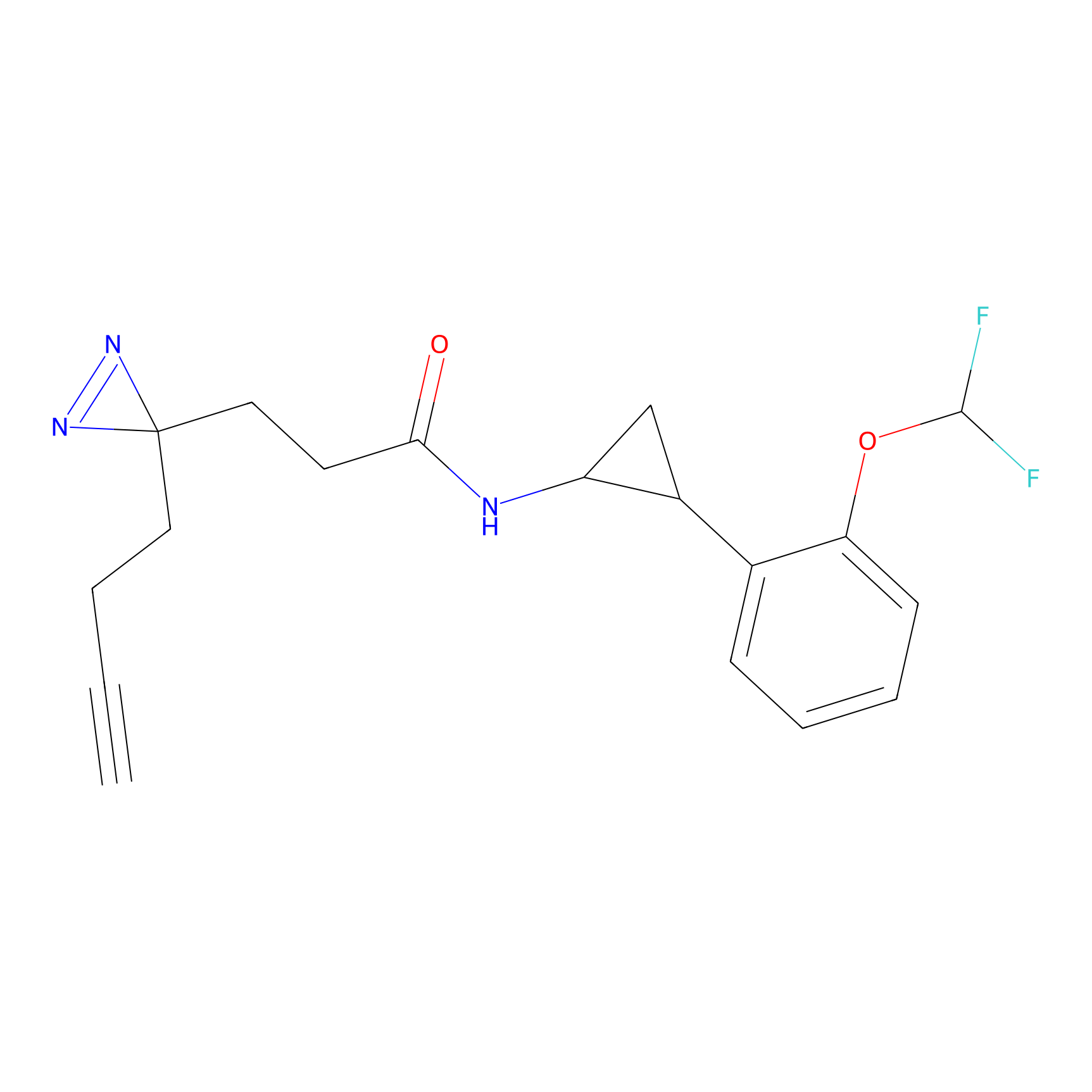
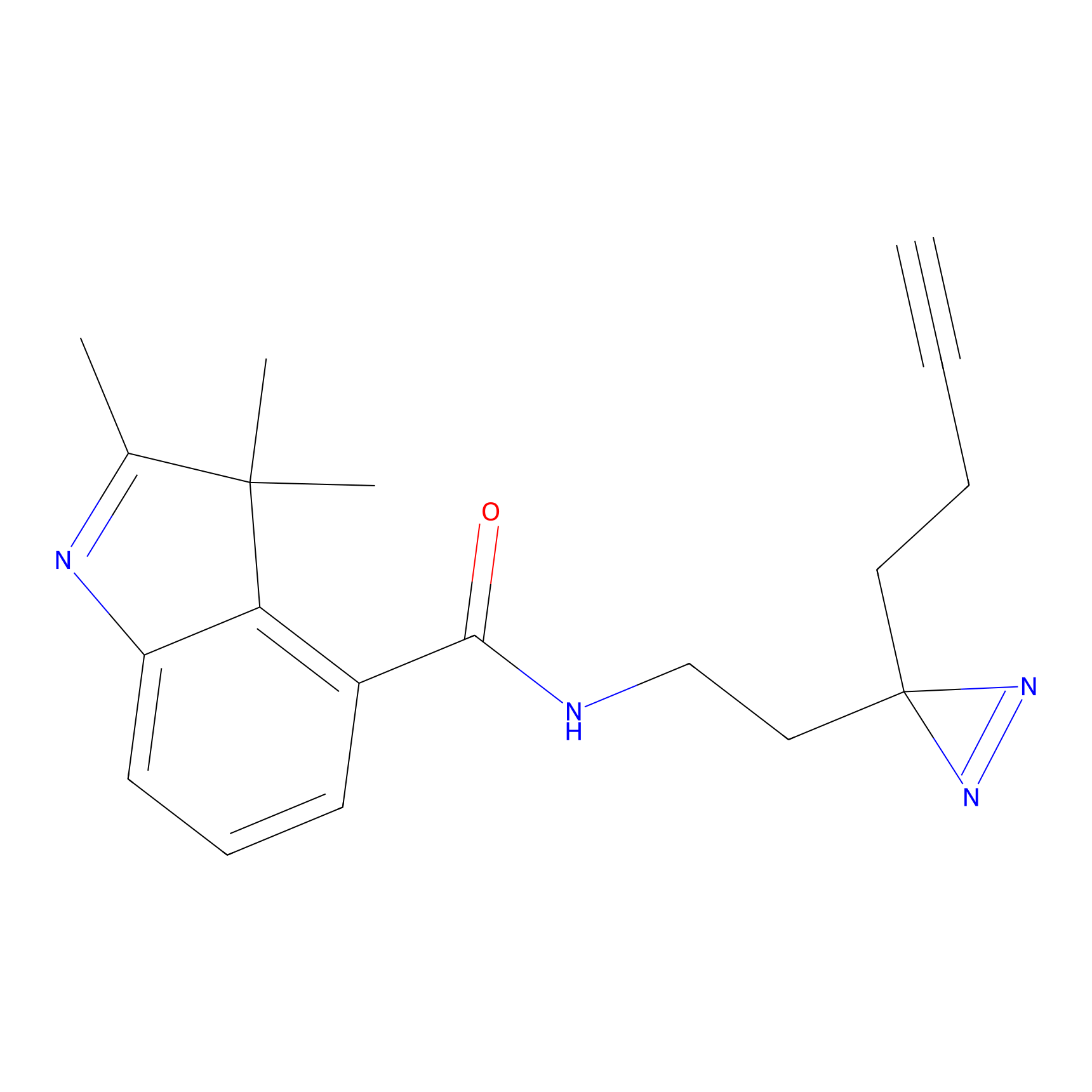
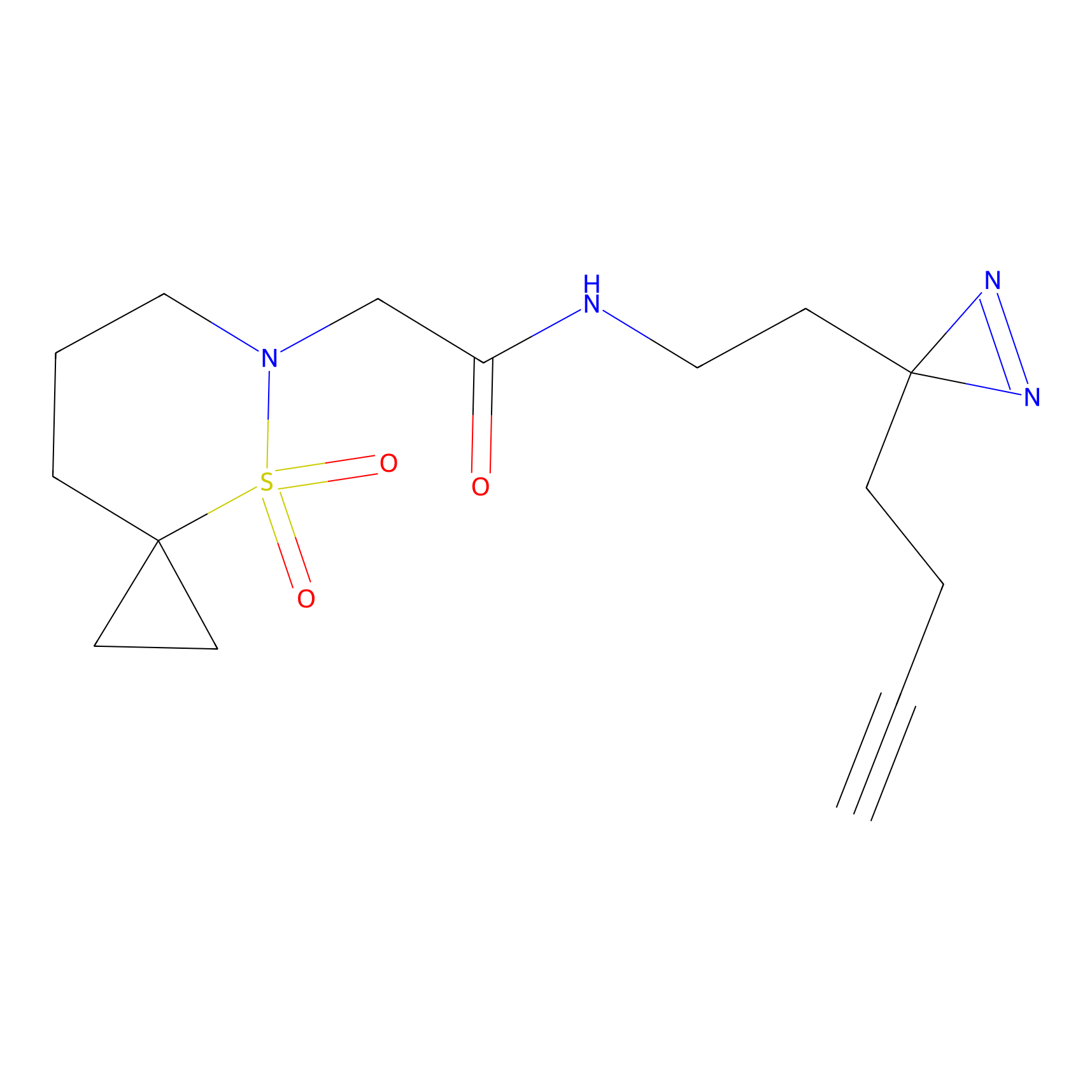
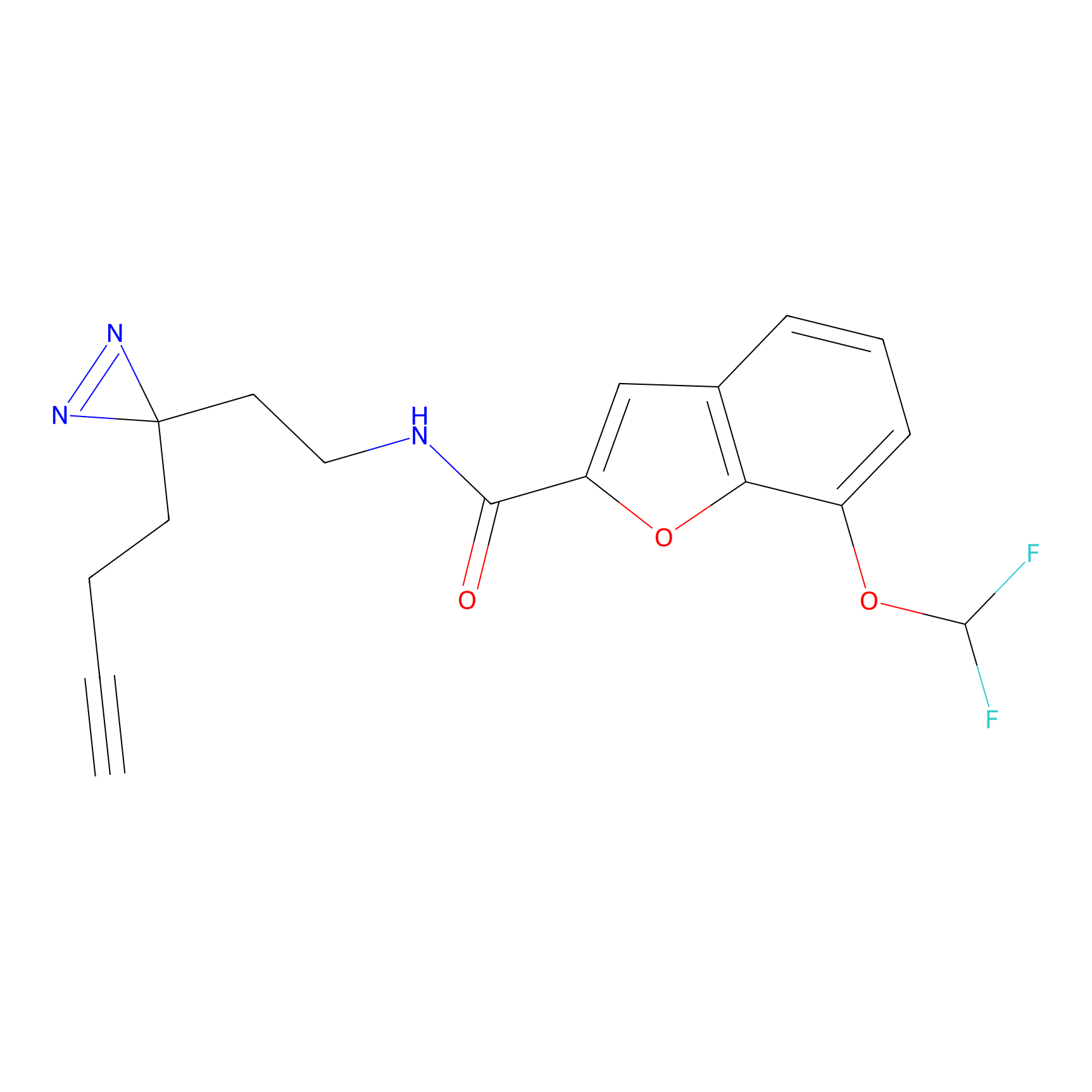
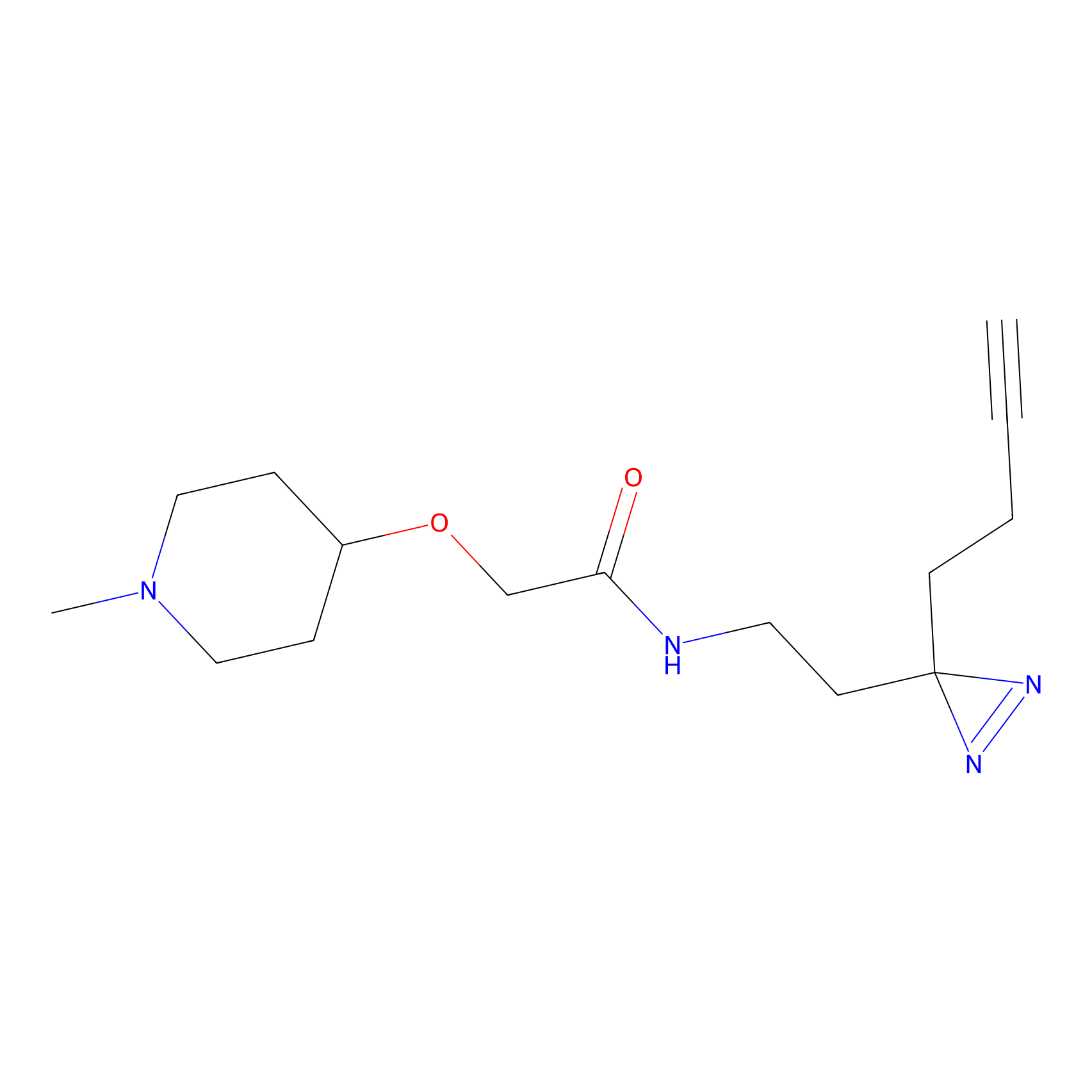
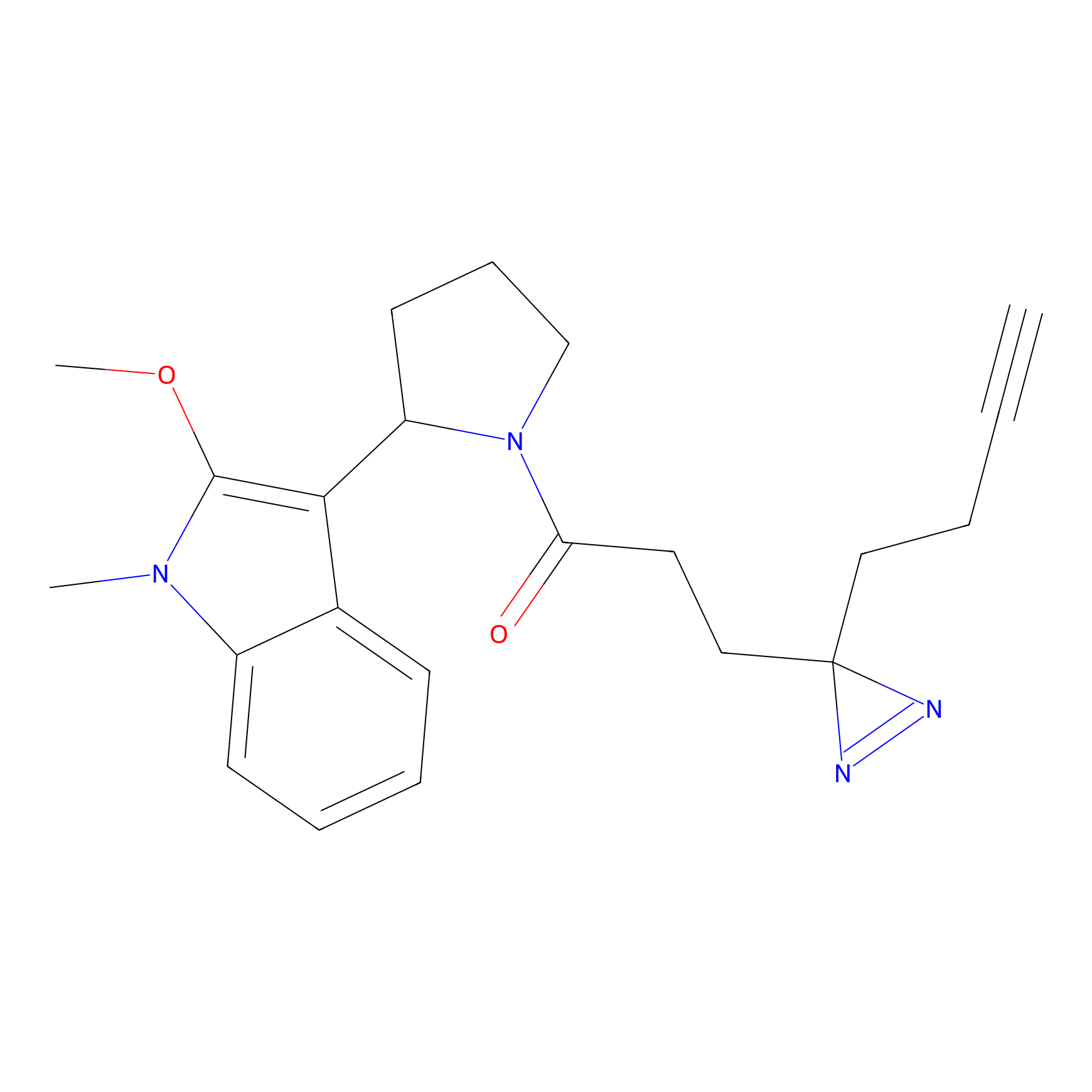
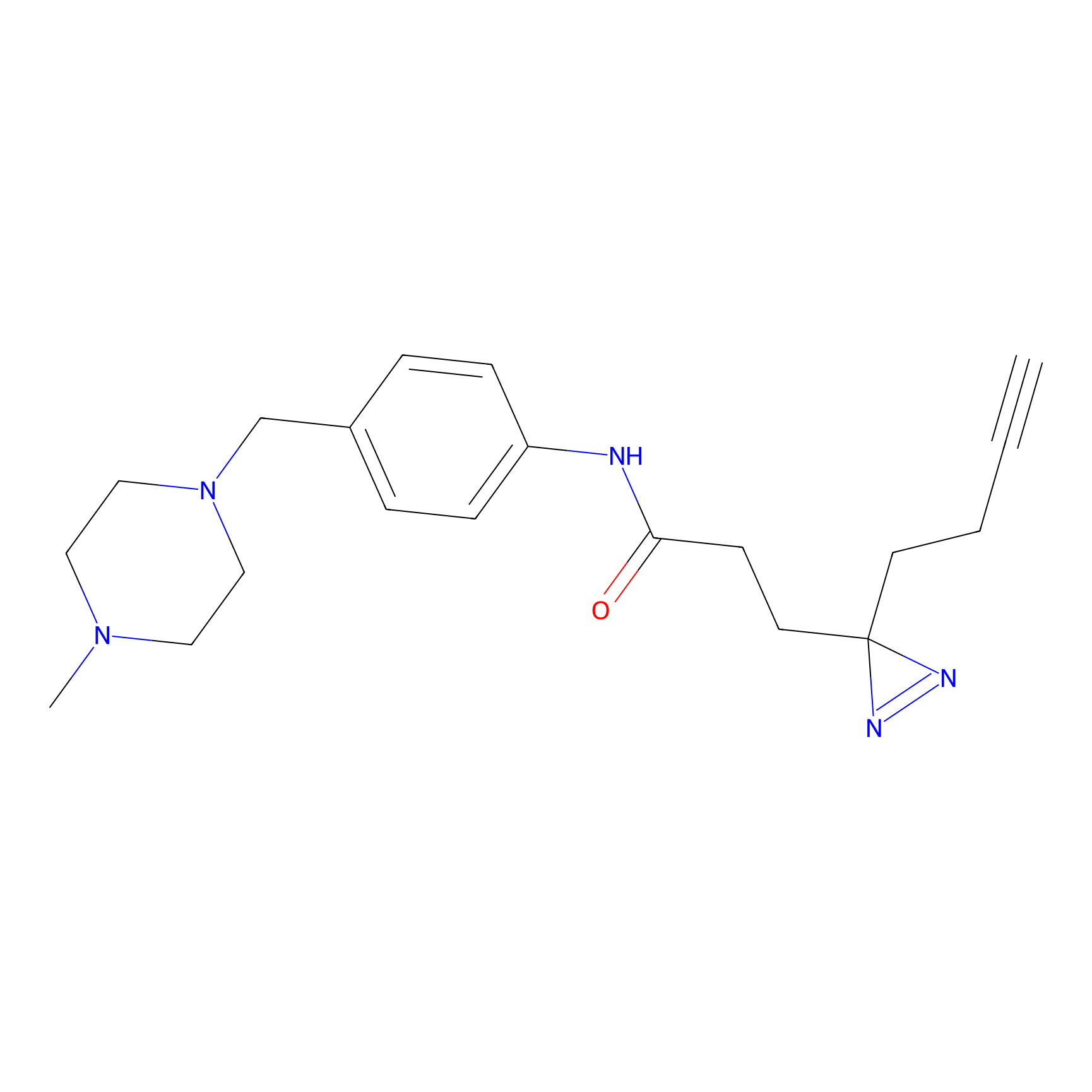
|
FBPP2 Probe Info |
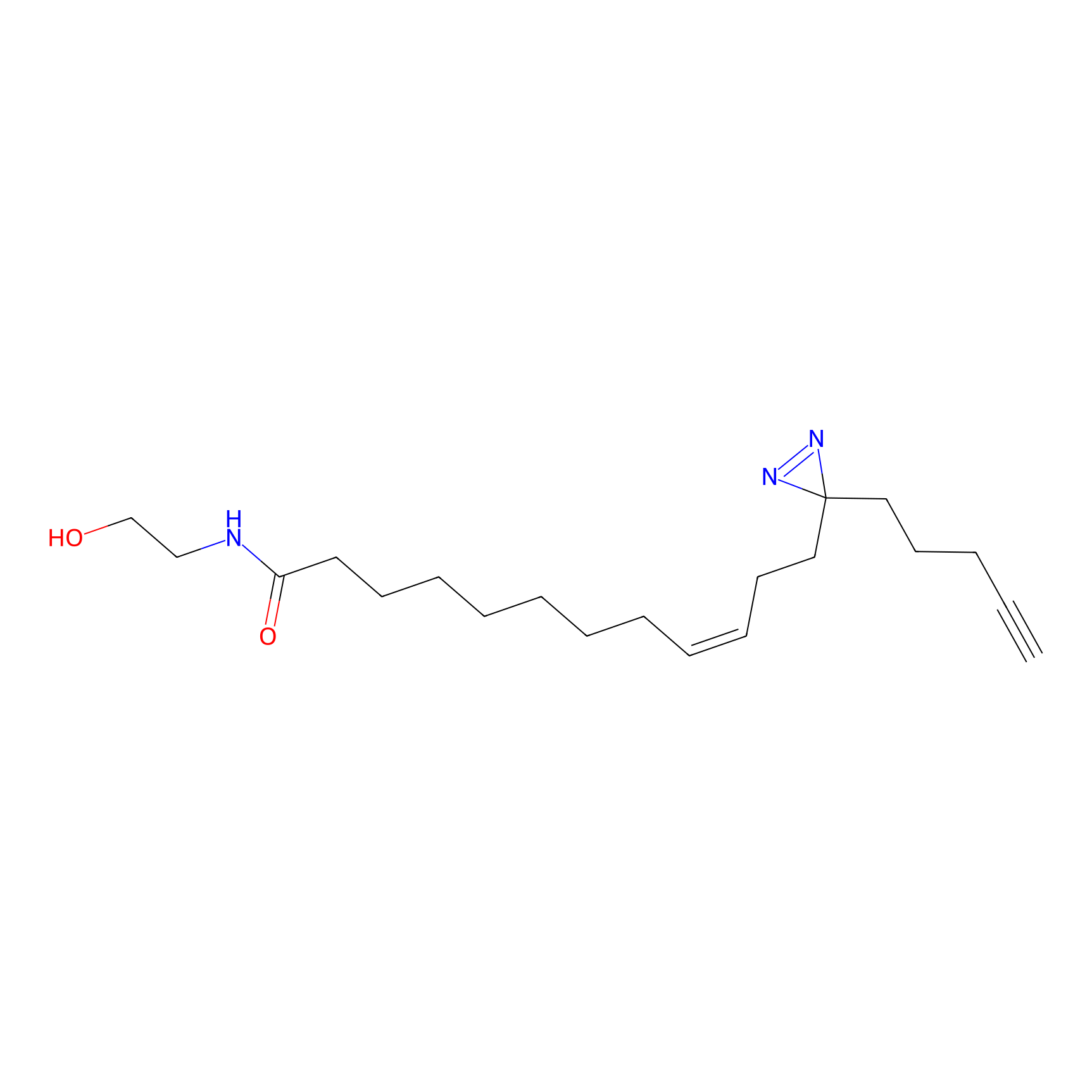
 |
6.64 | LDD0318 | [1] | |
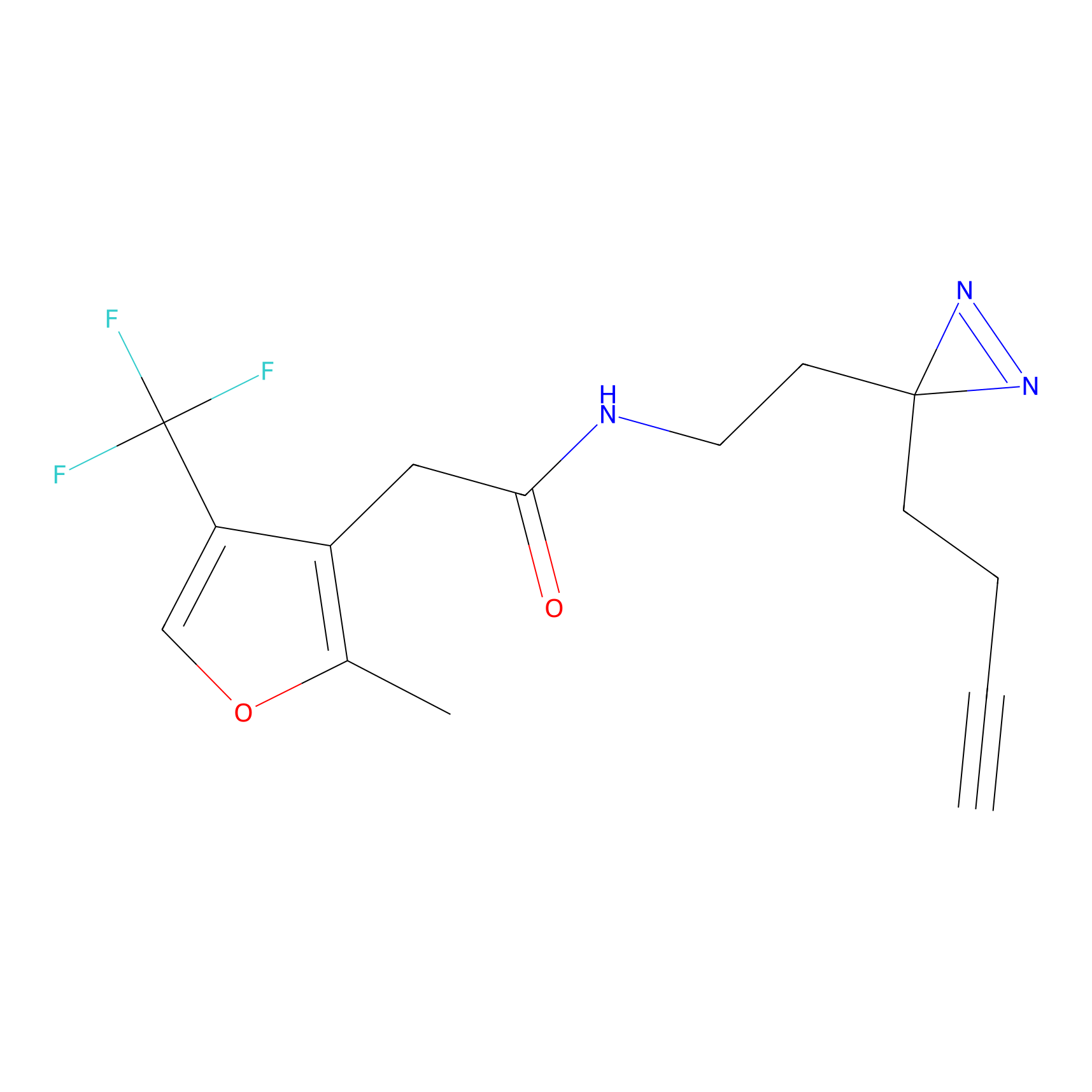
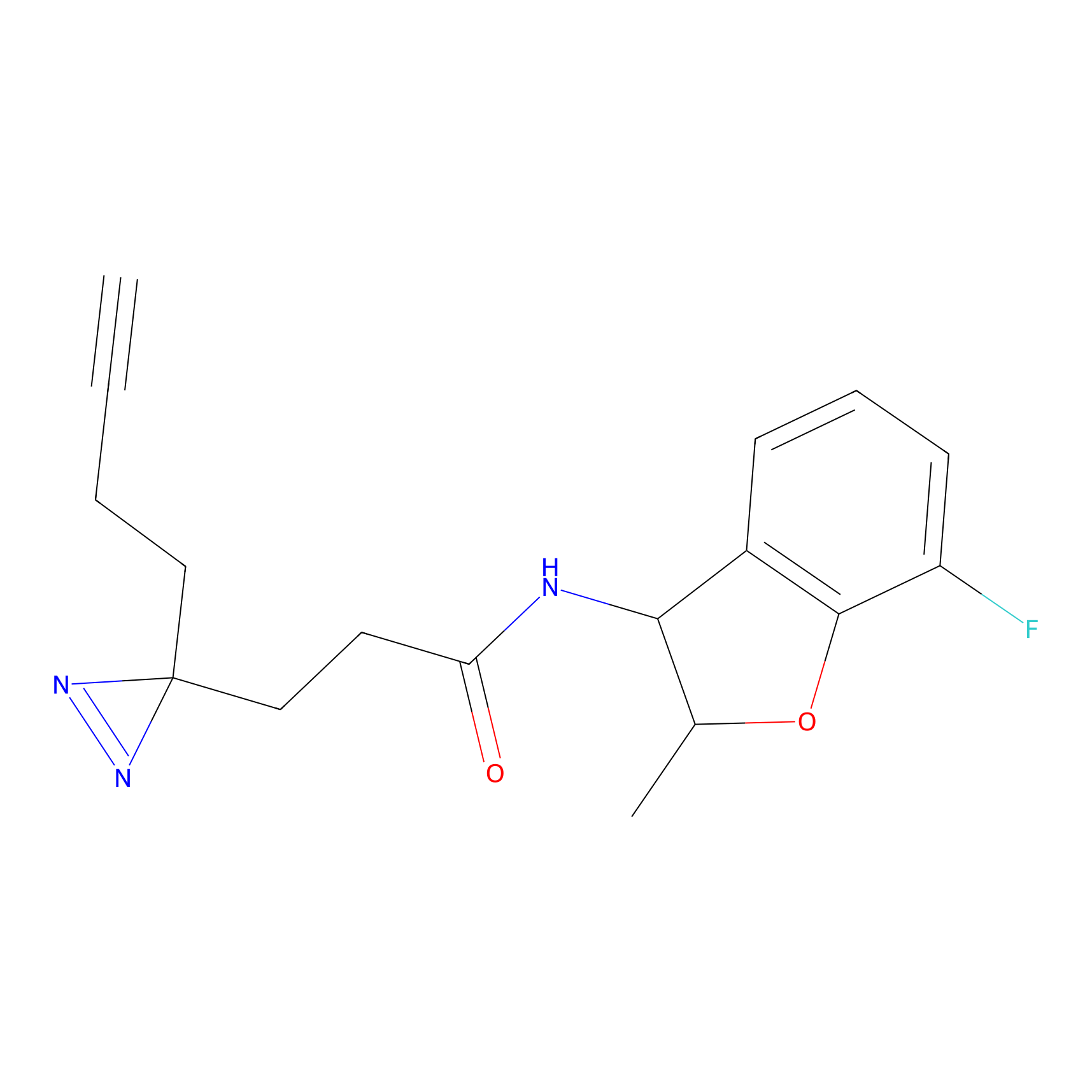
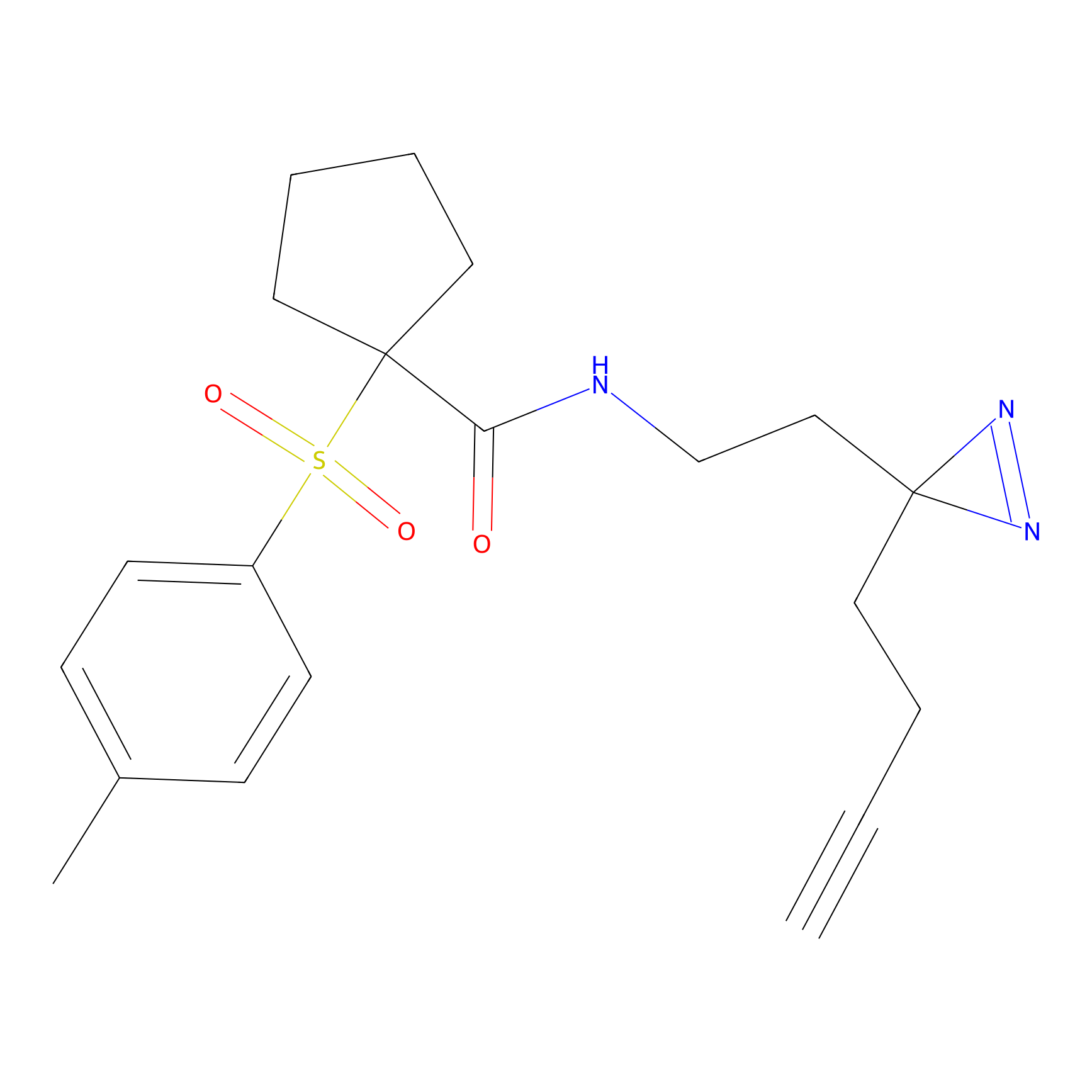
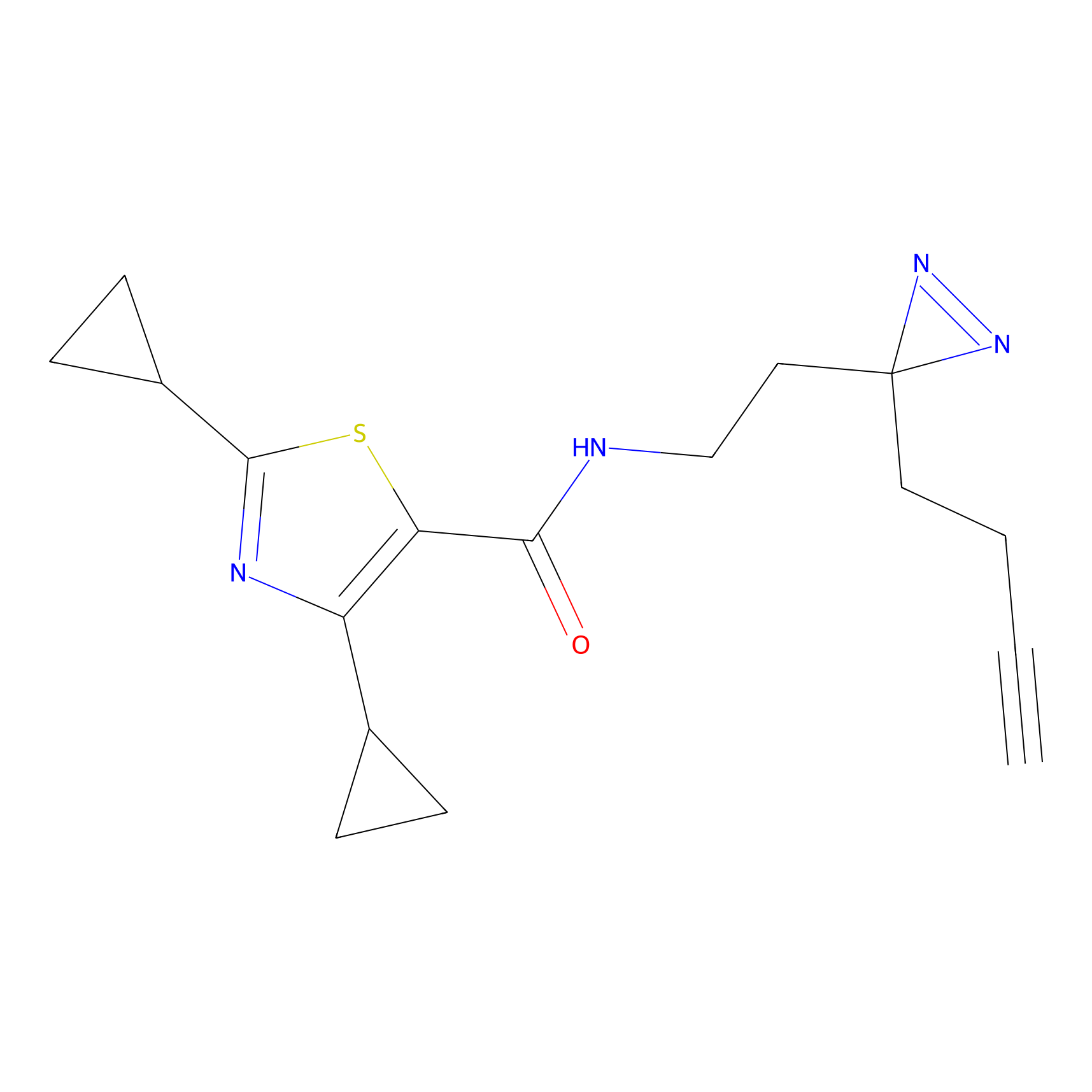
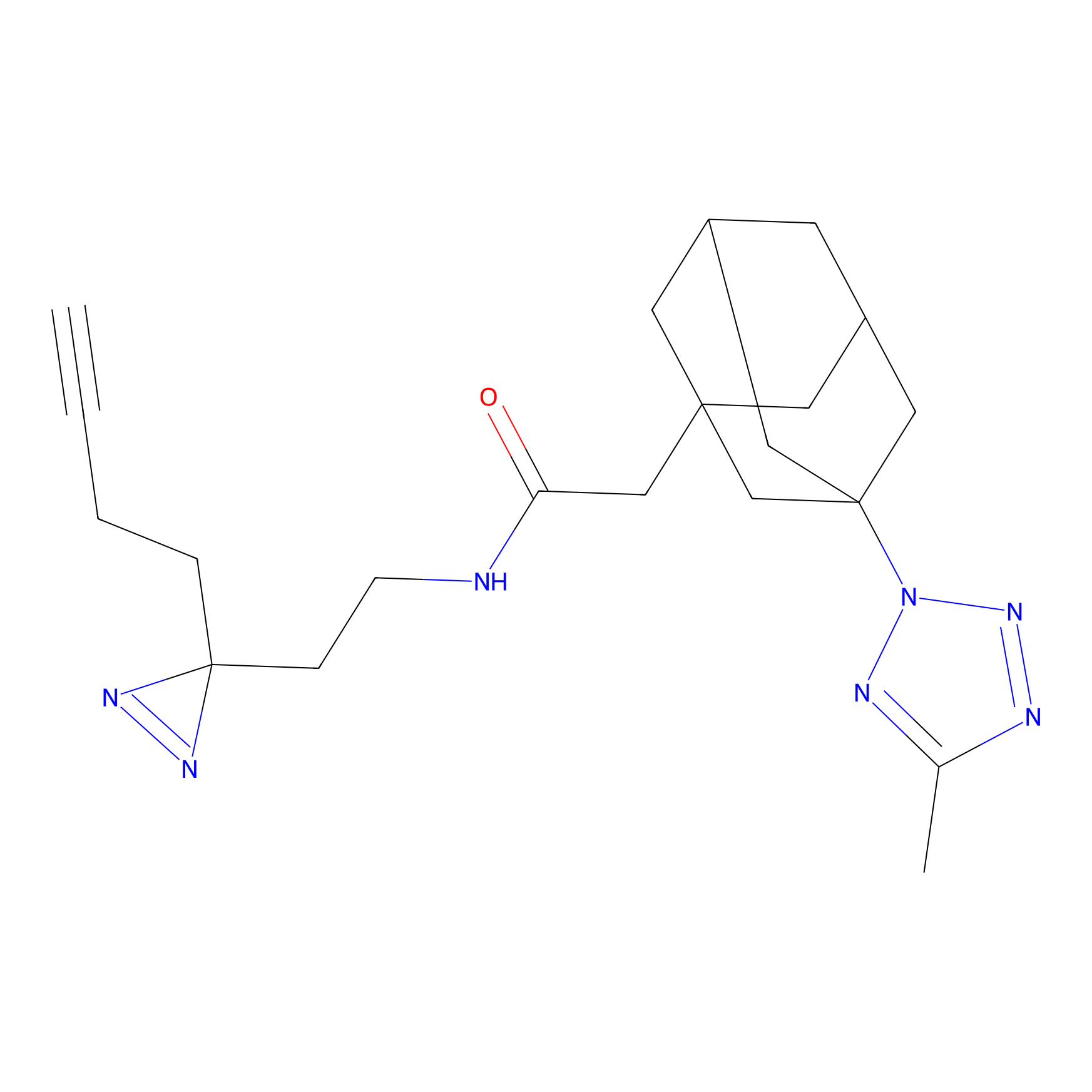
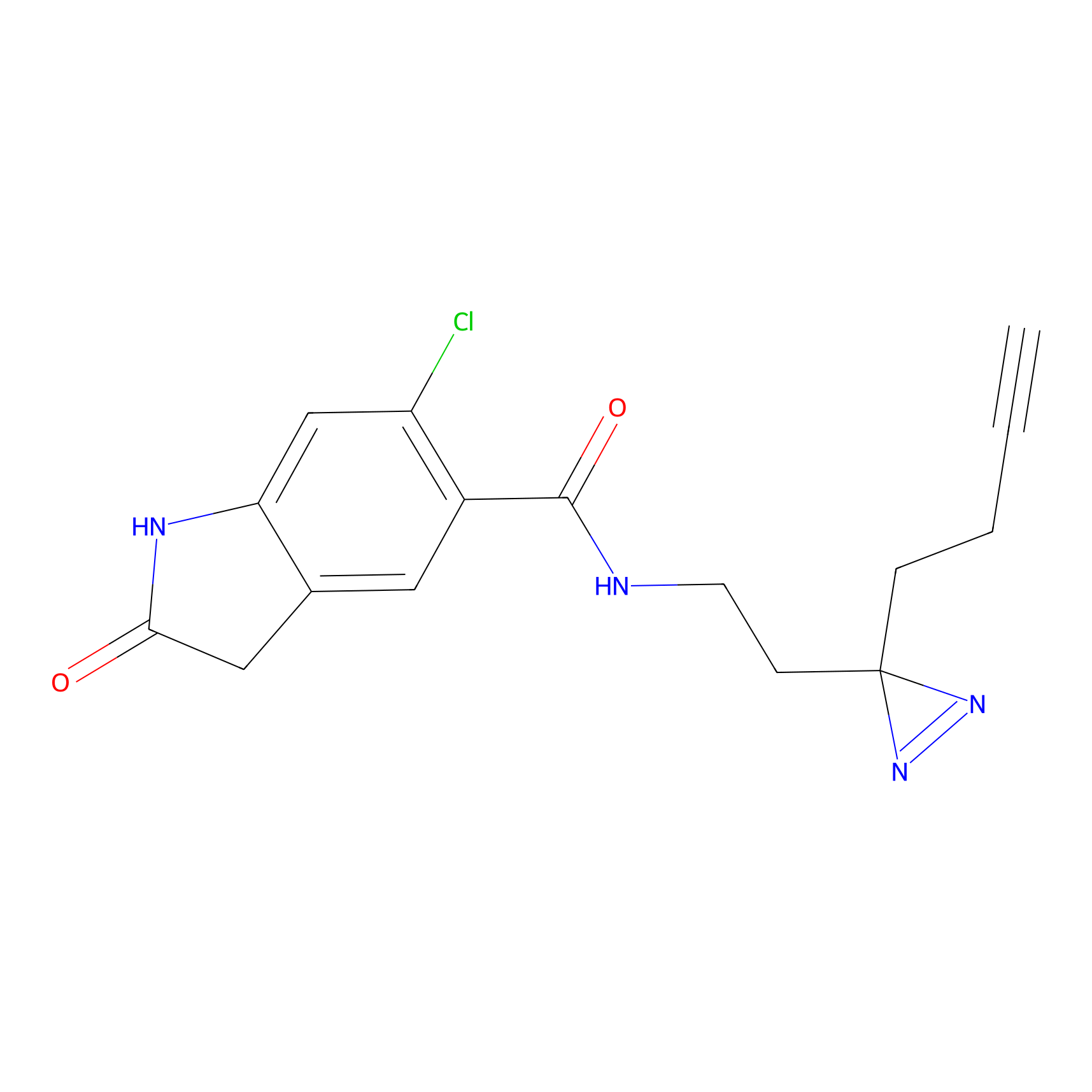
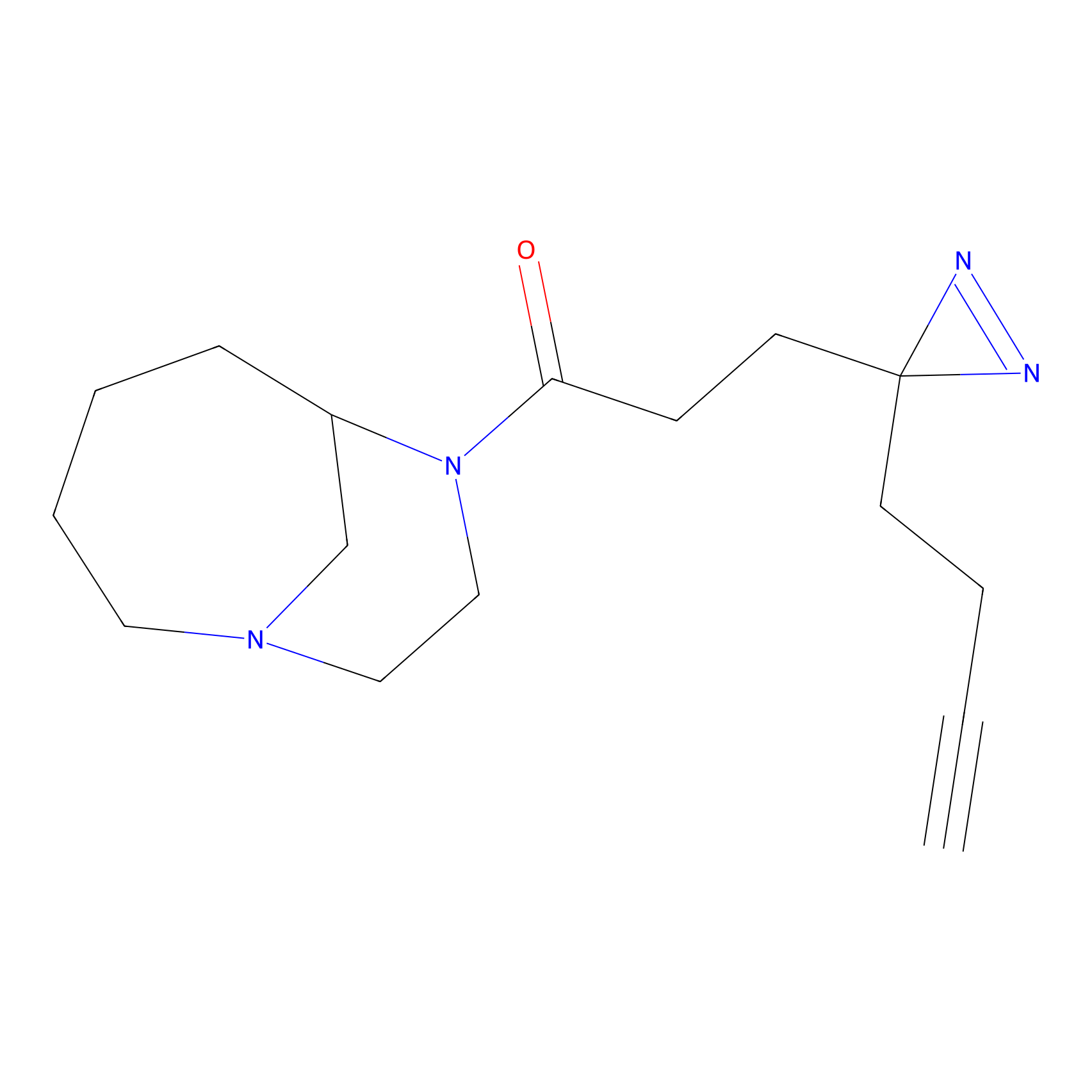
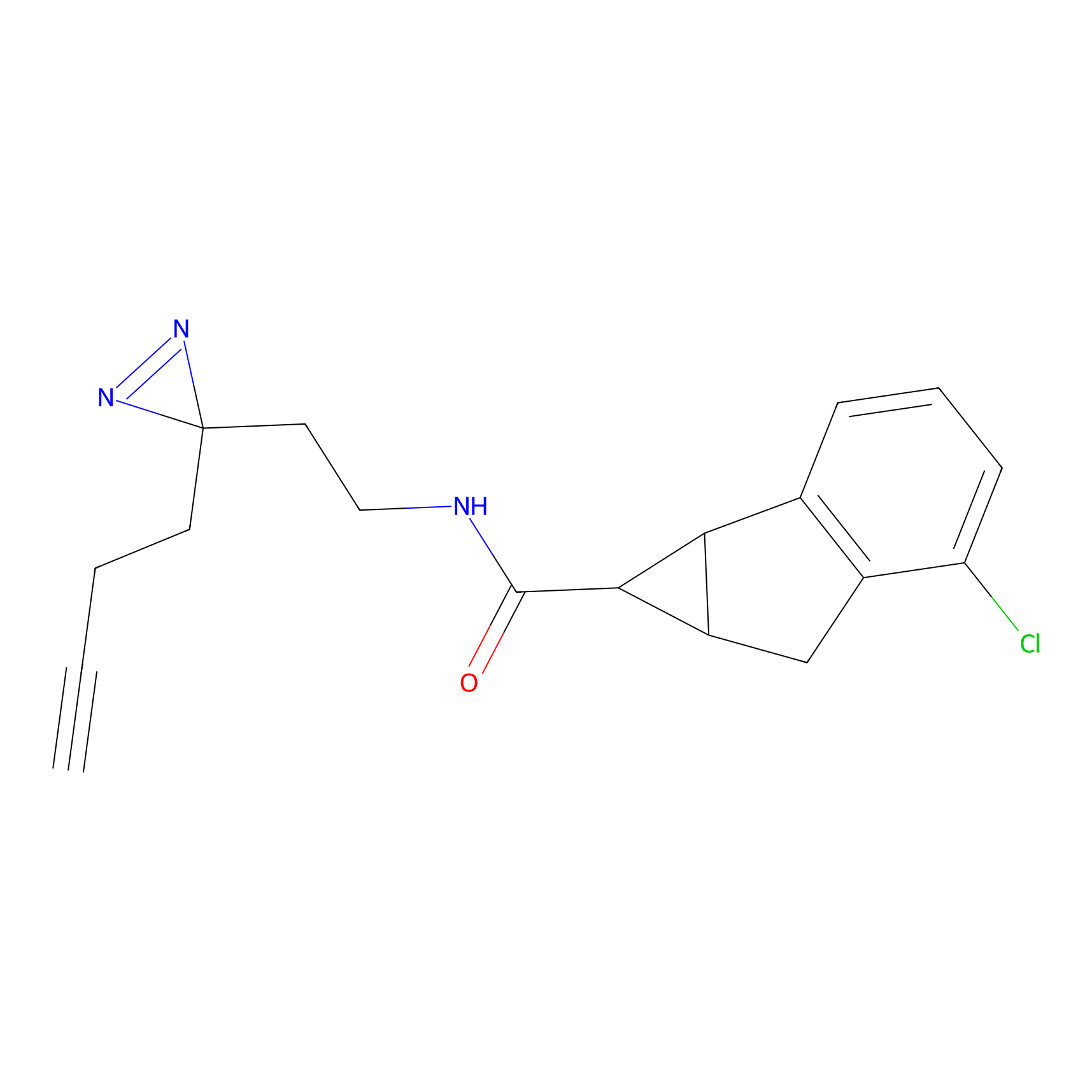
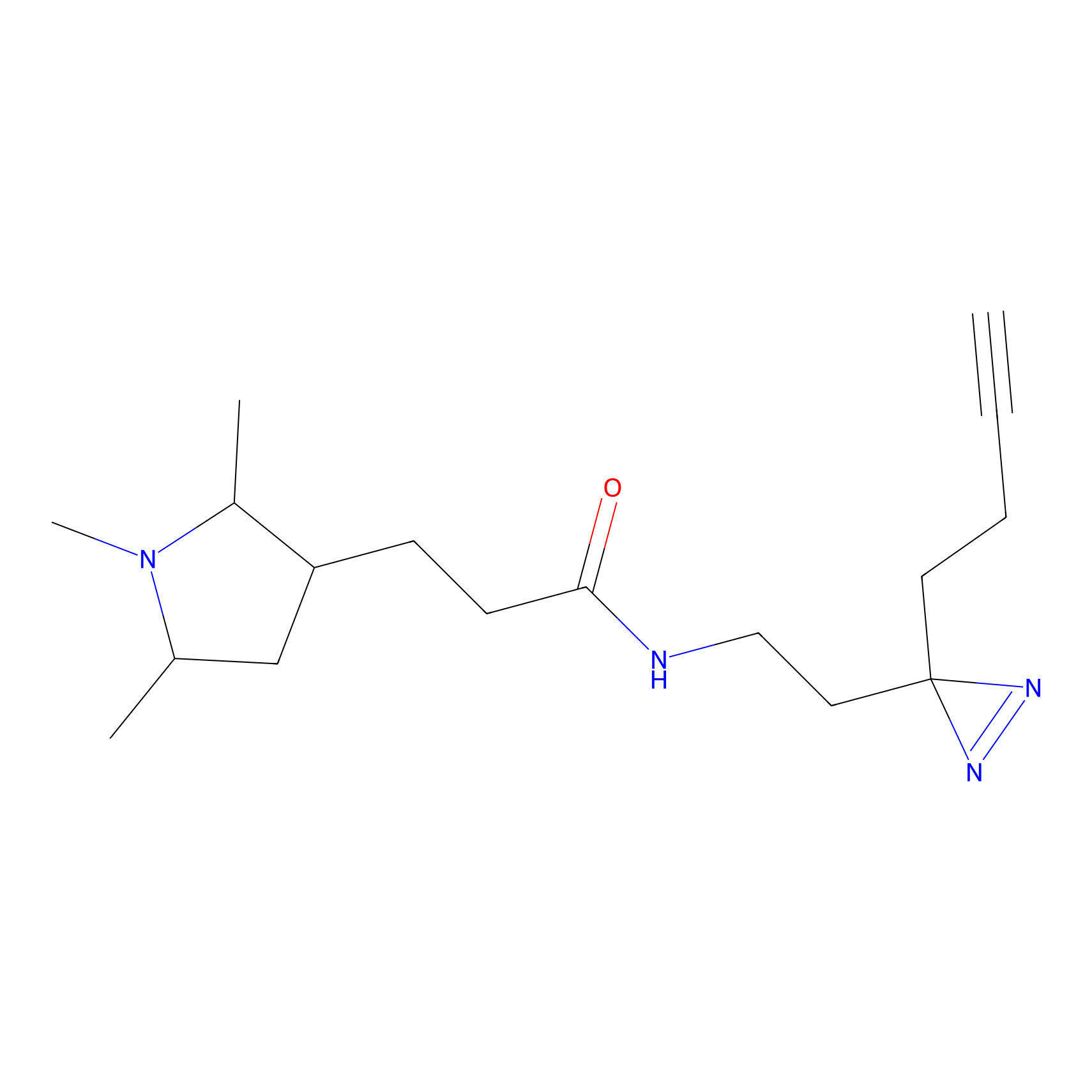
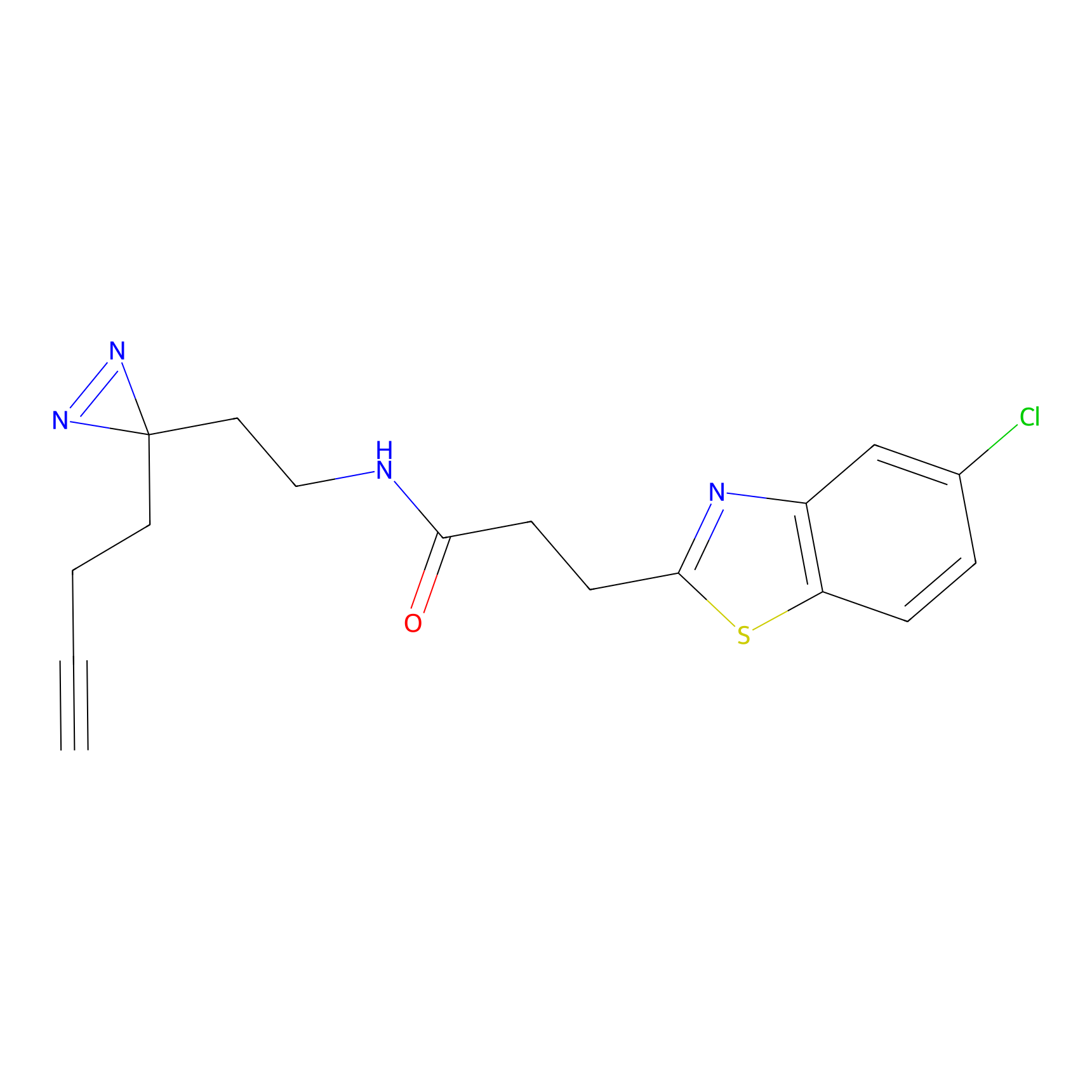
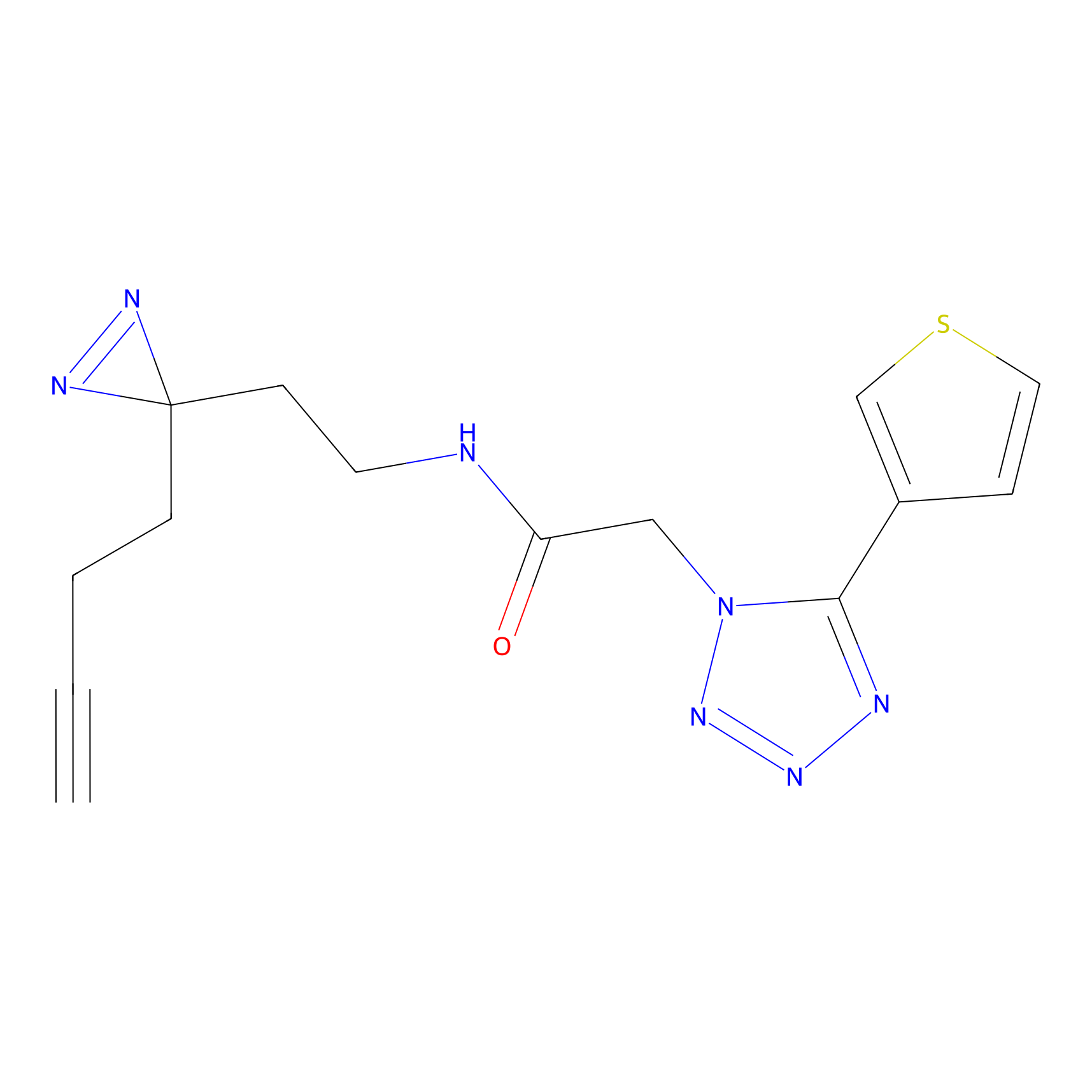
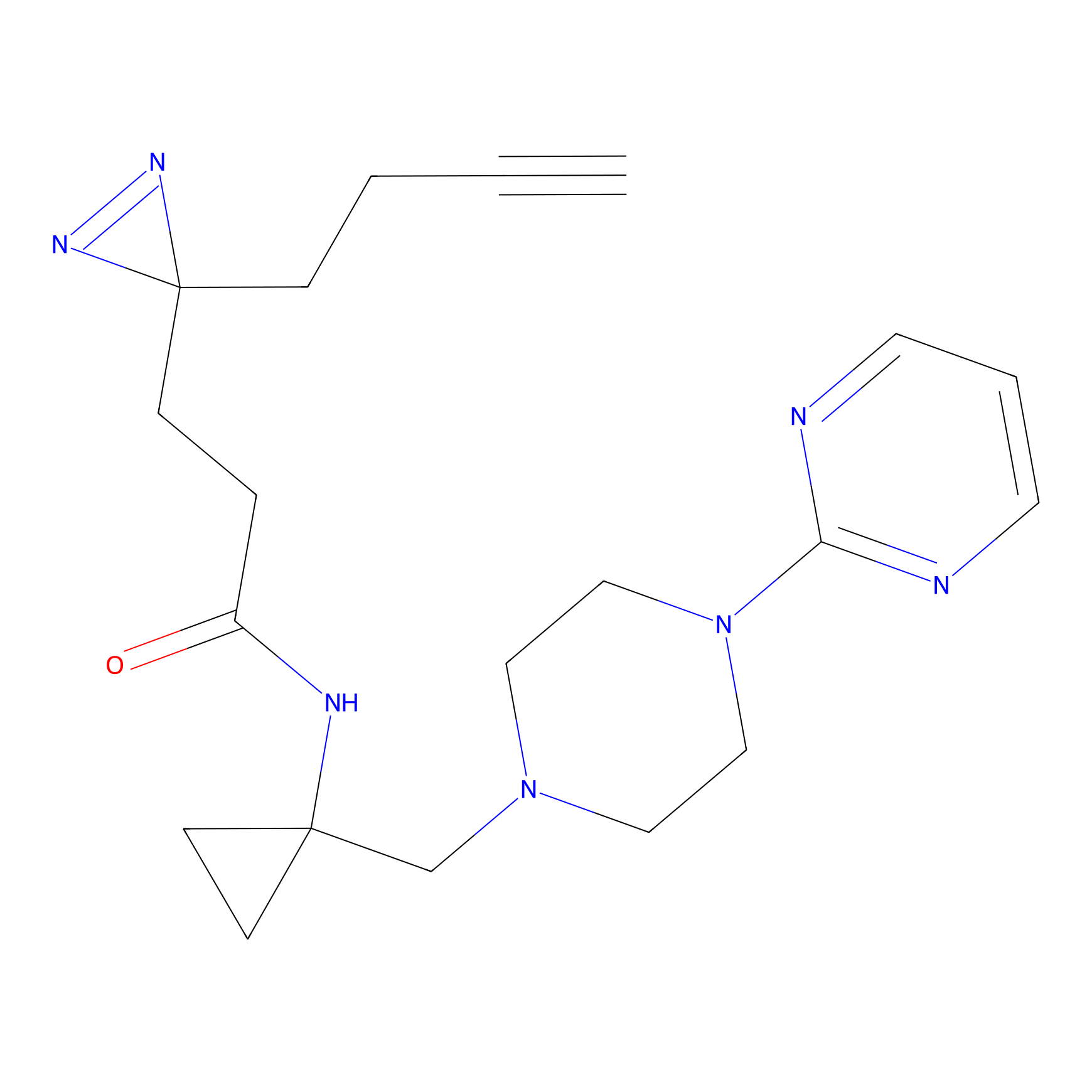
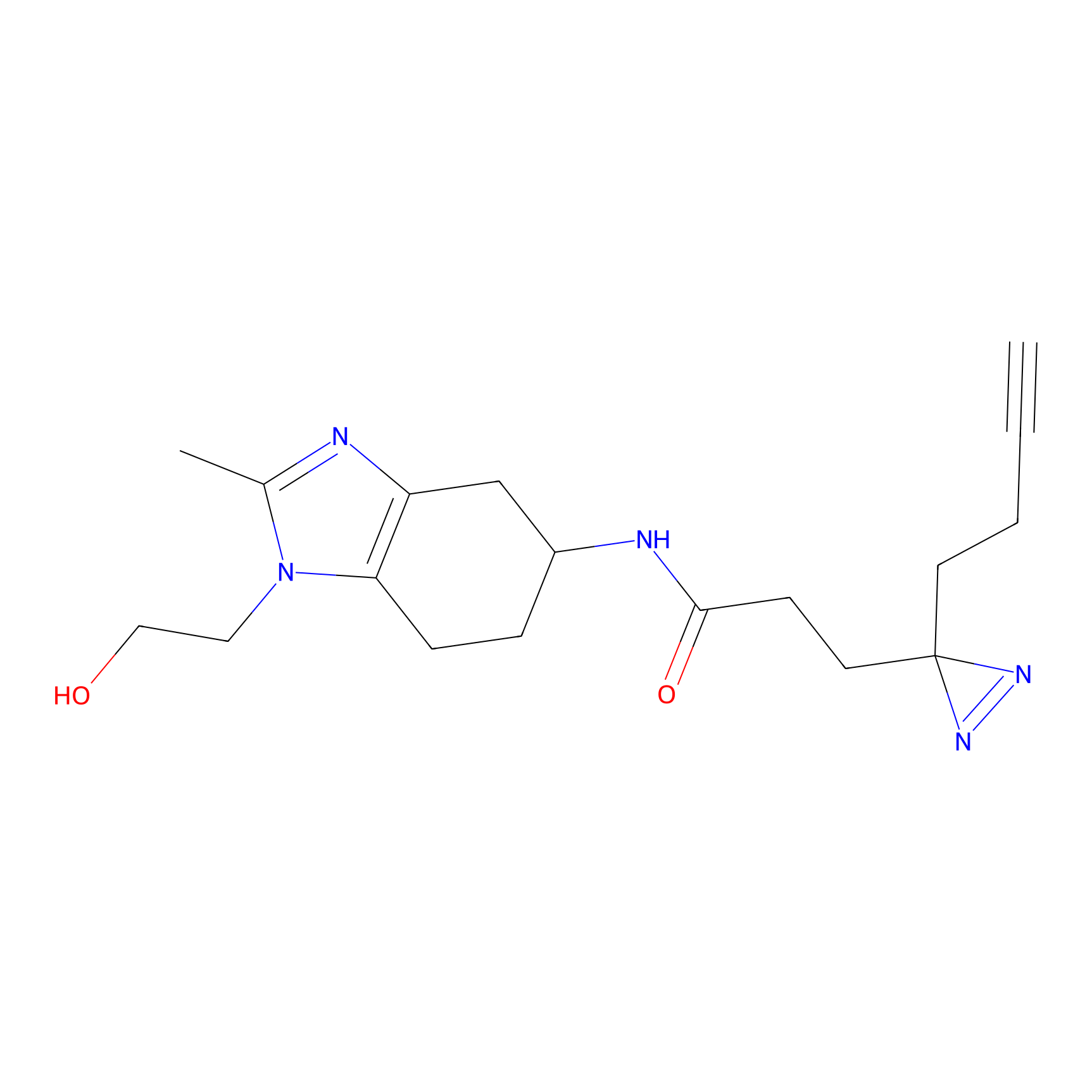
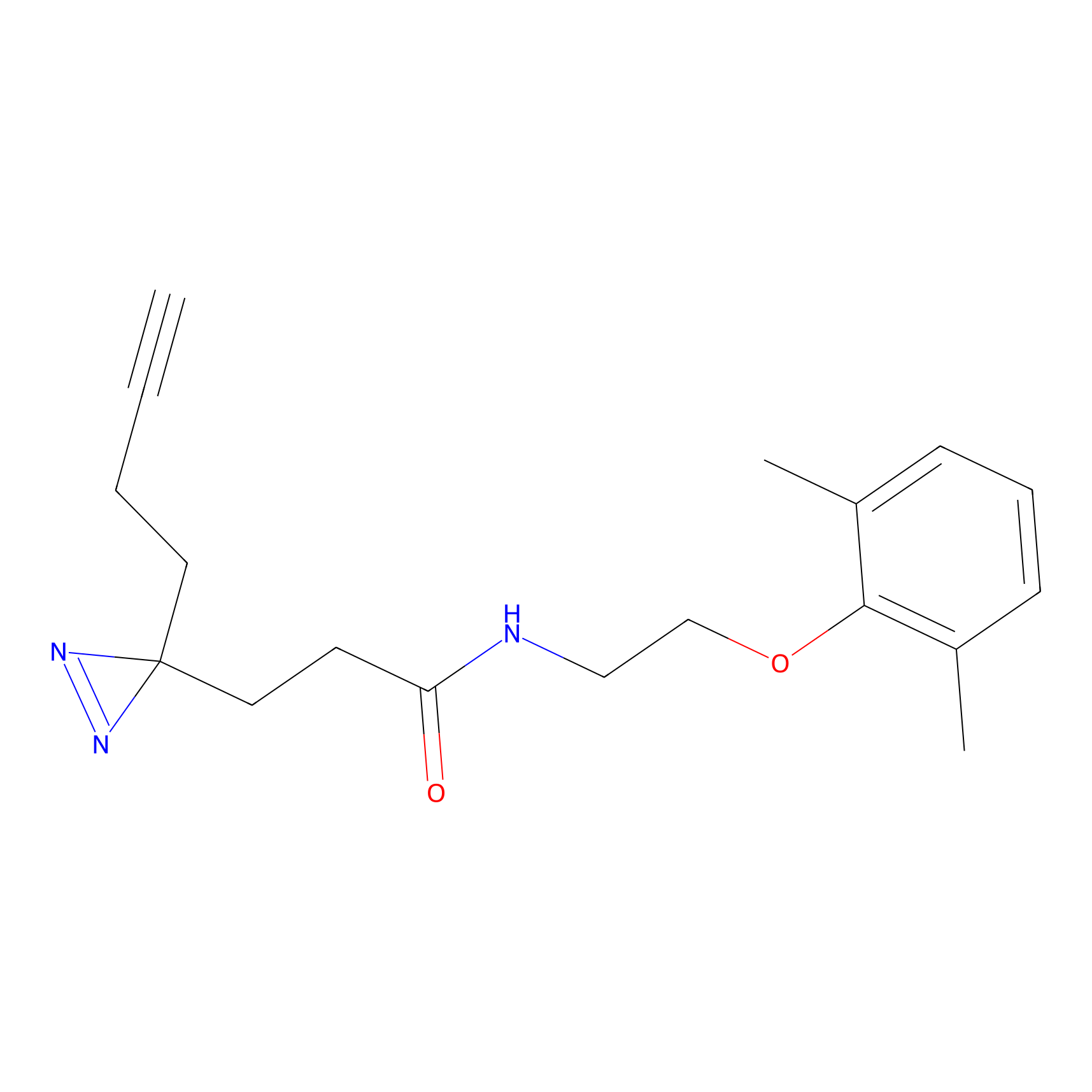
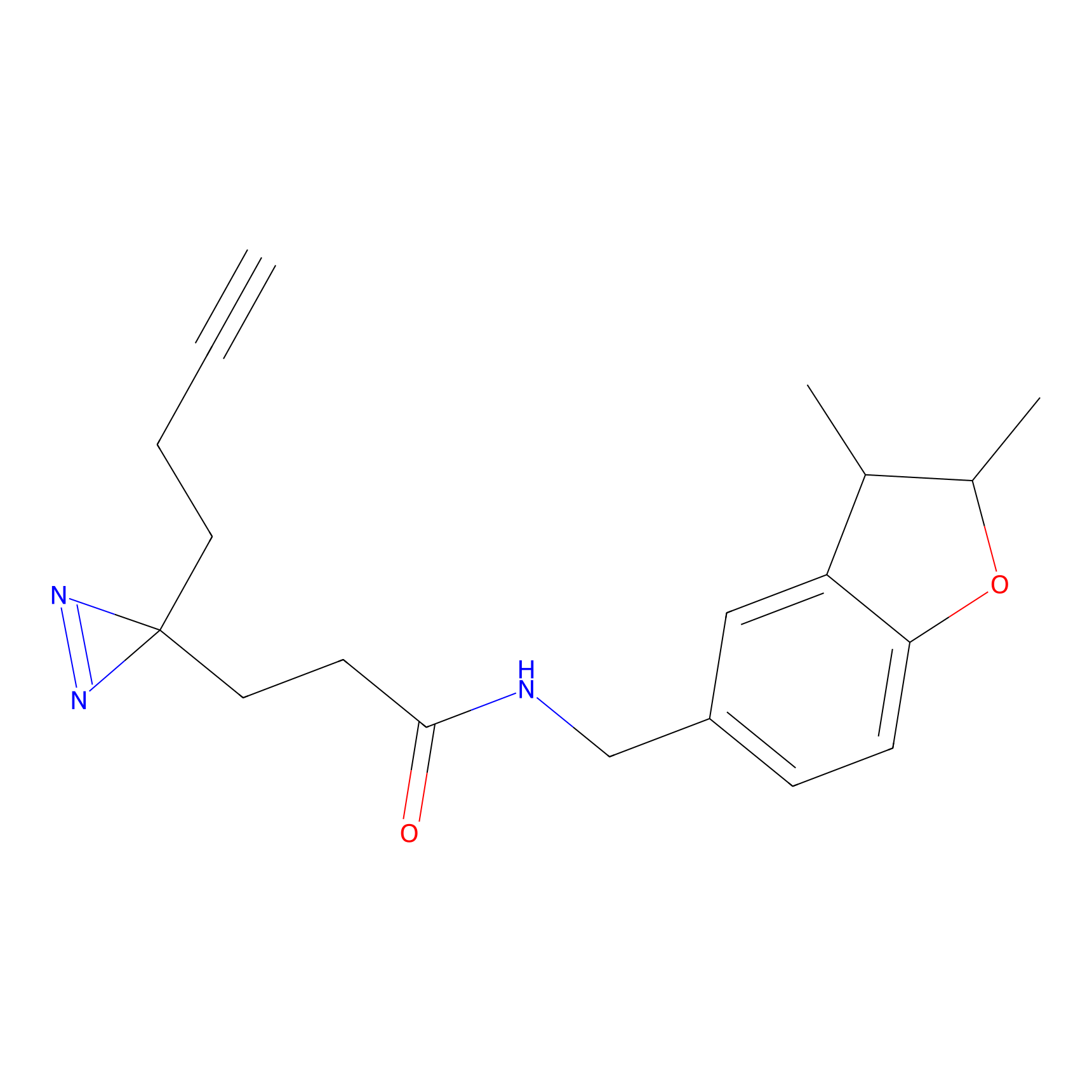
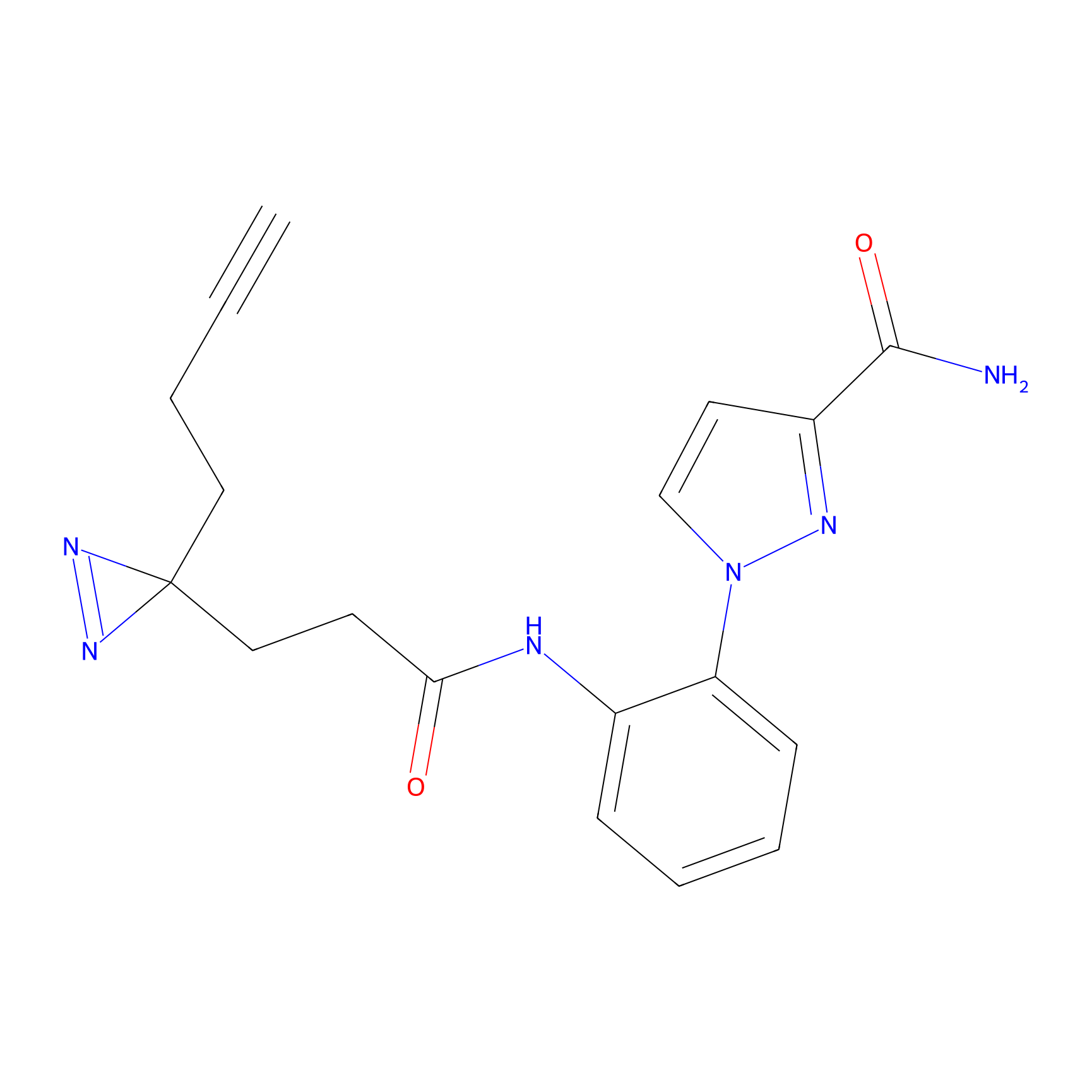
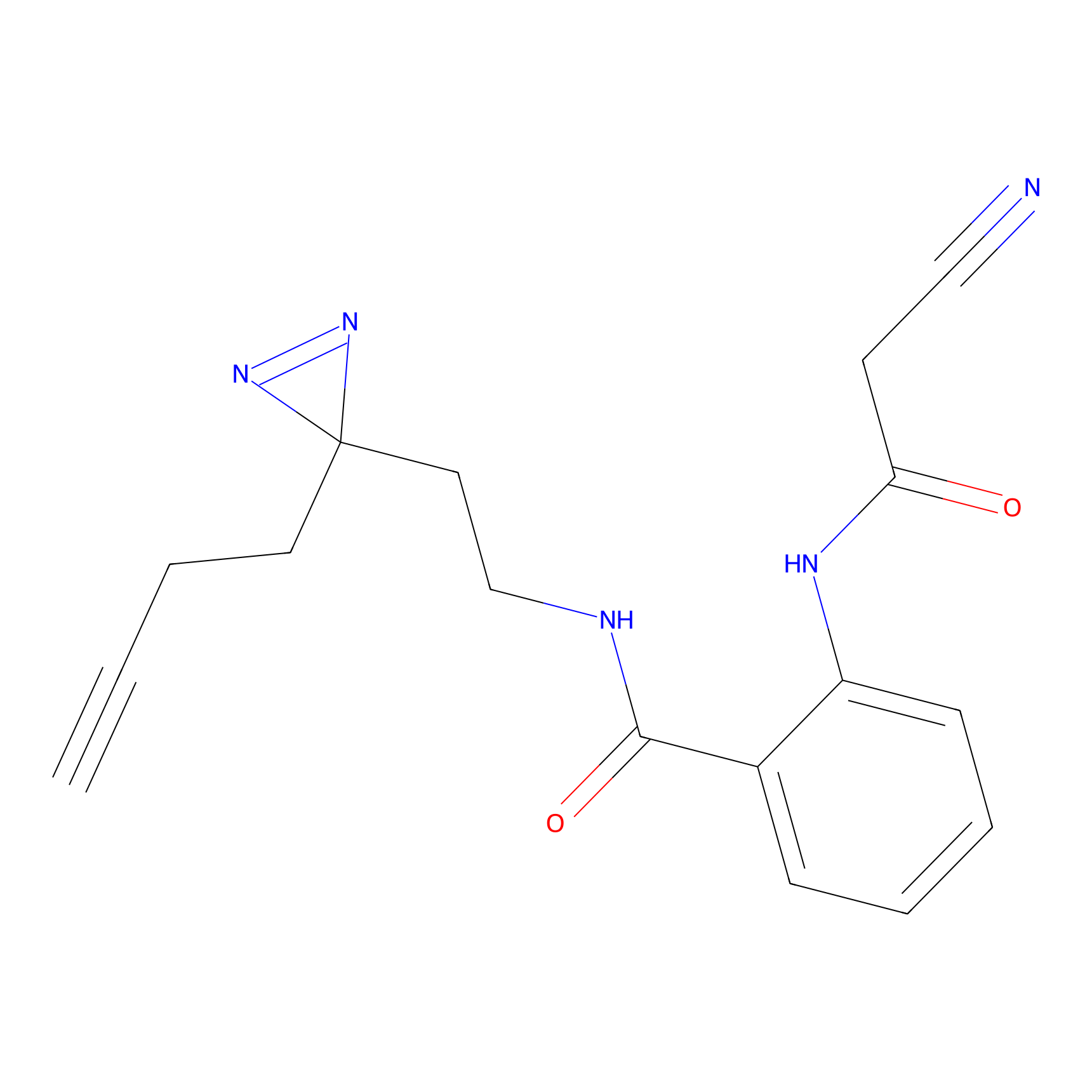
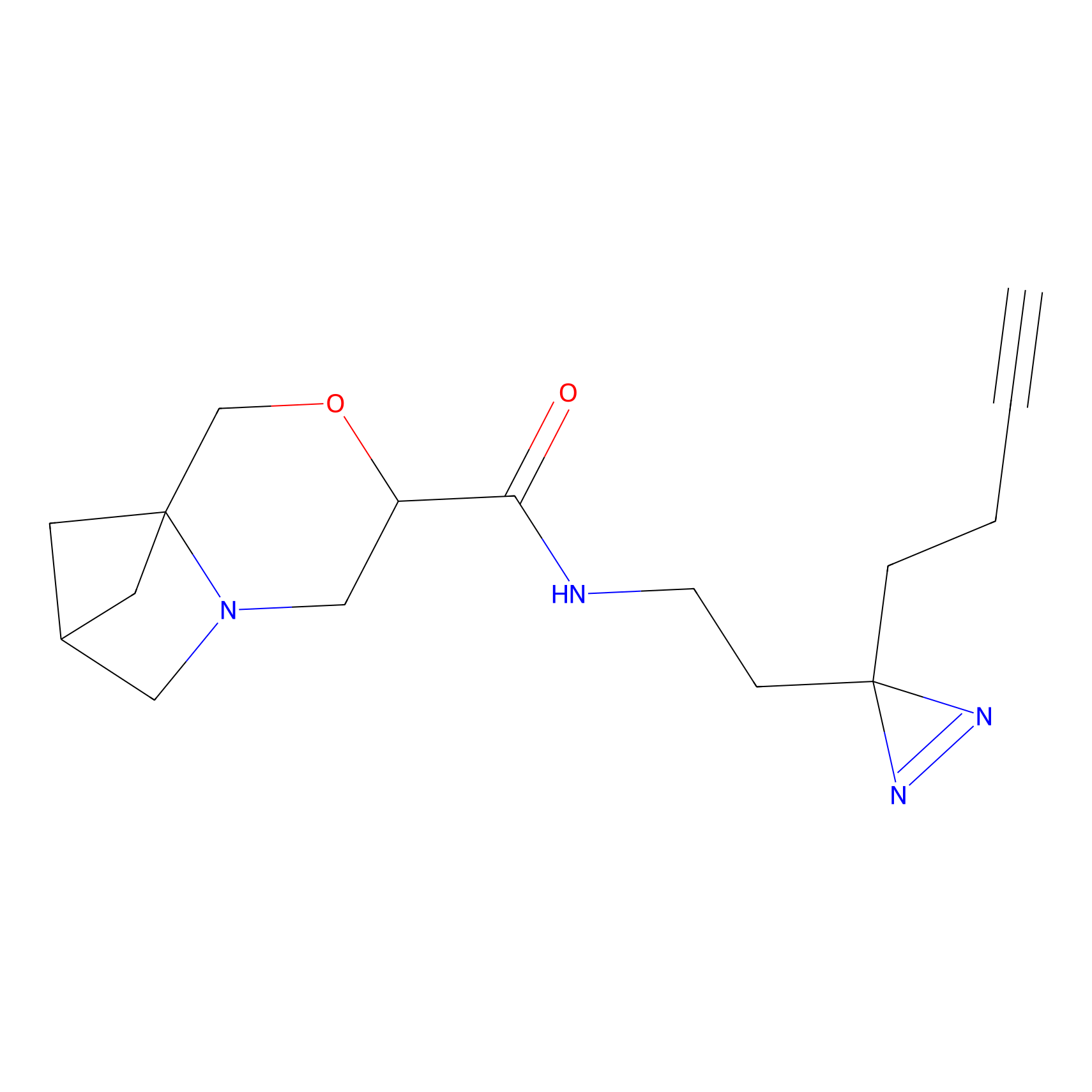
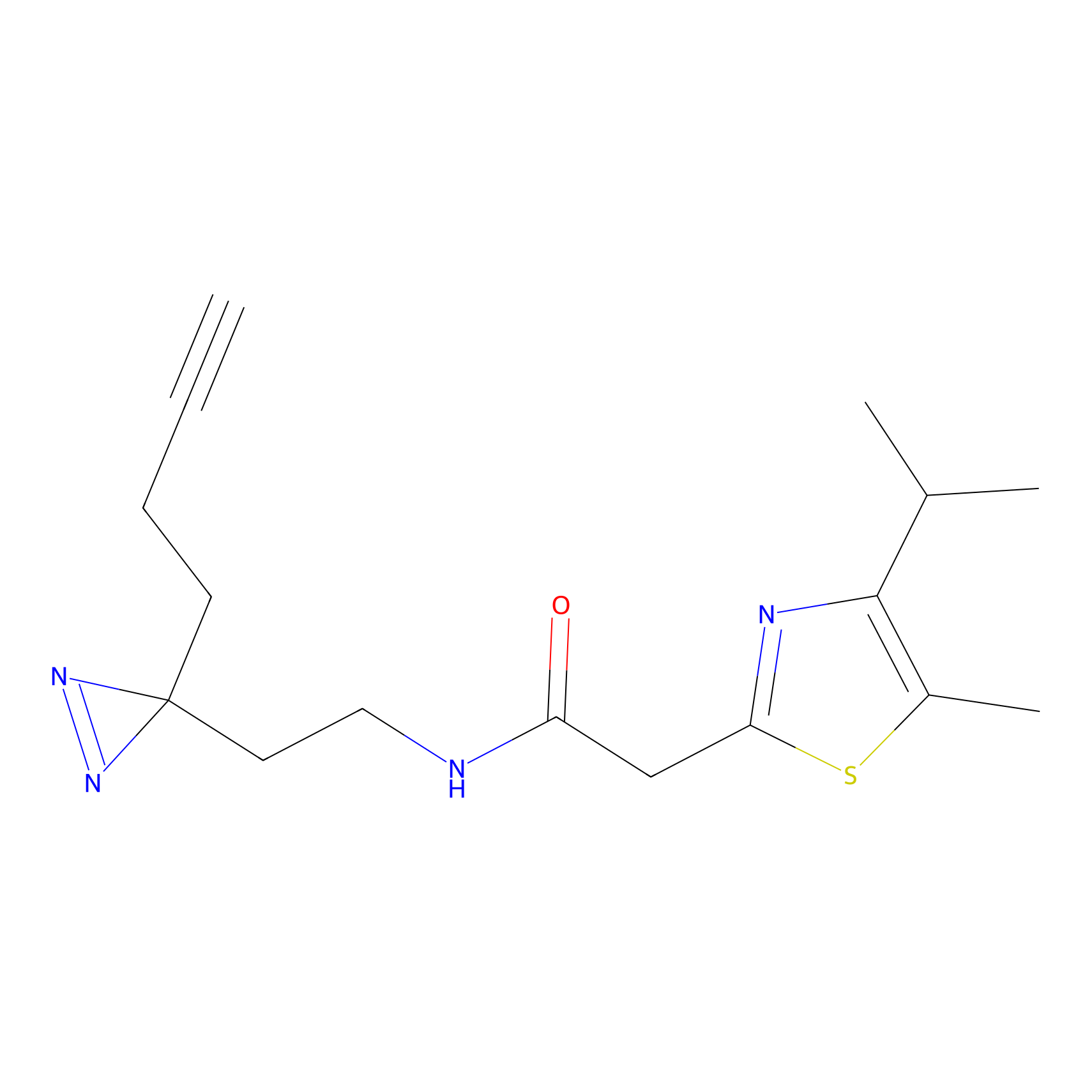
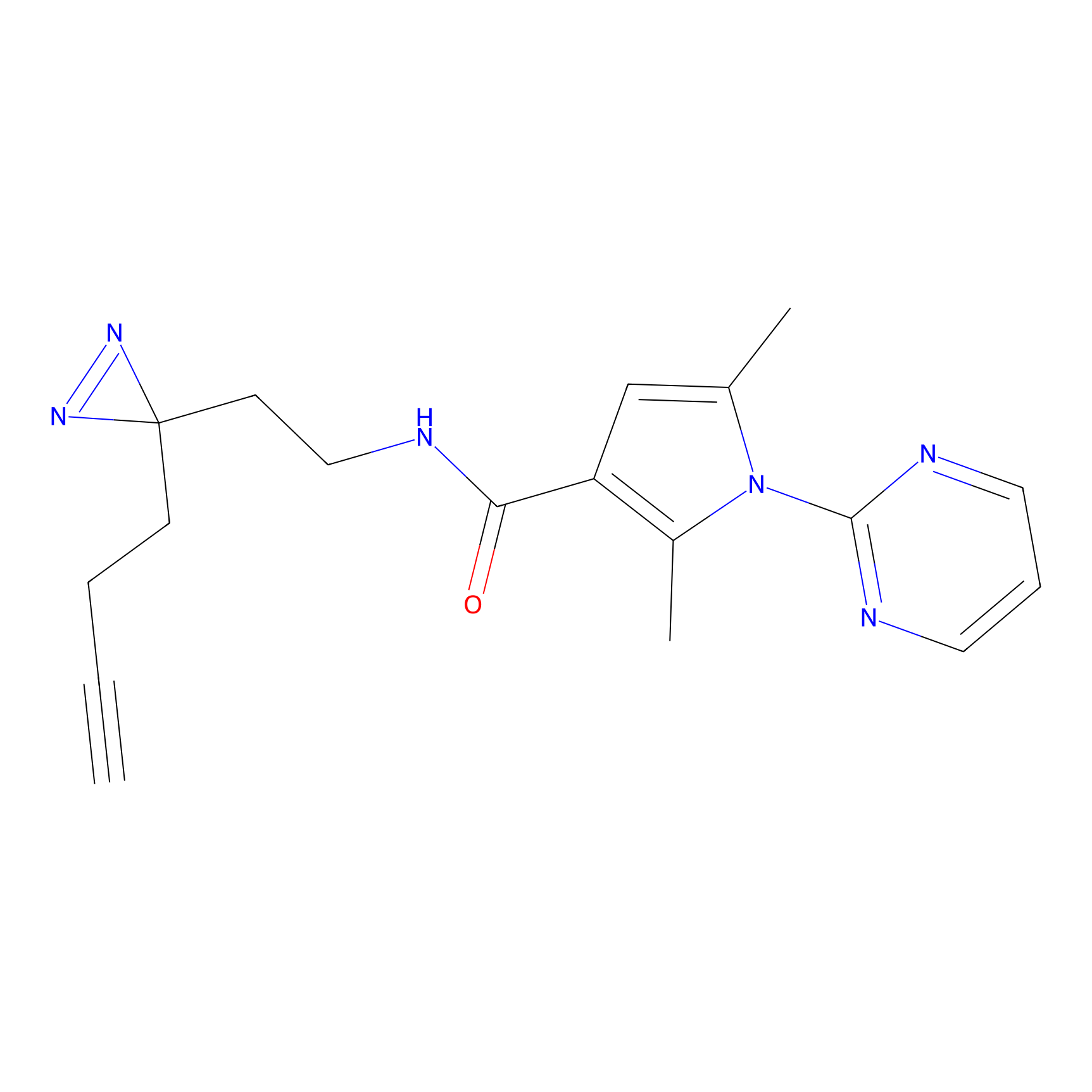
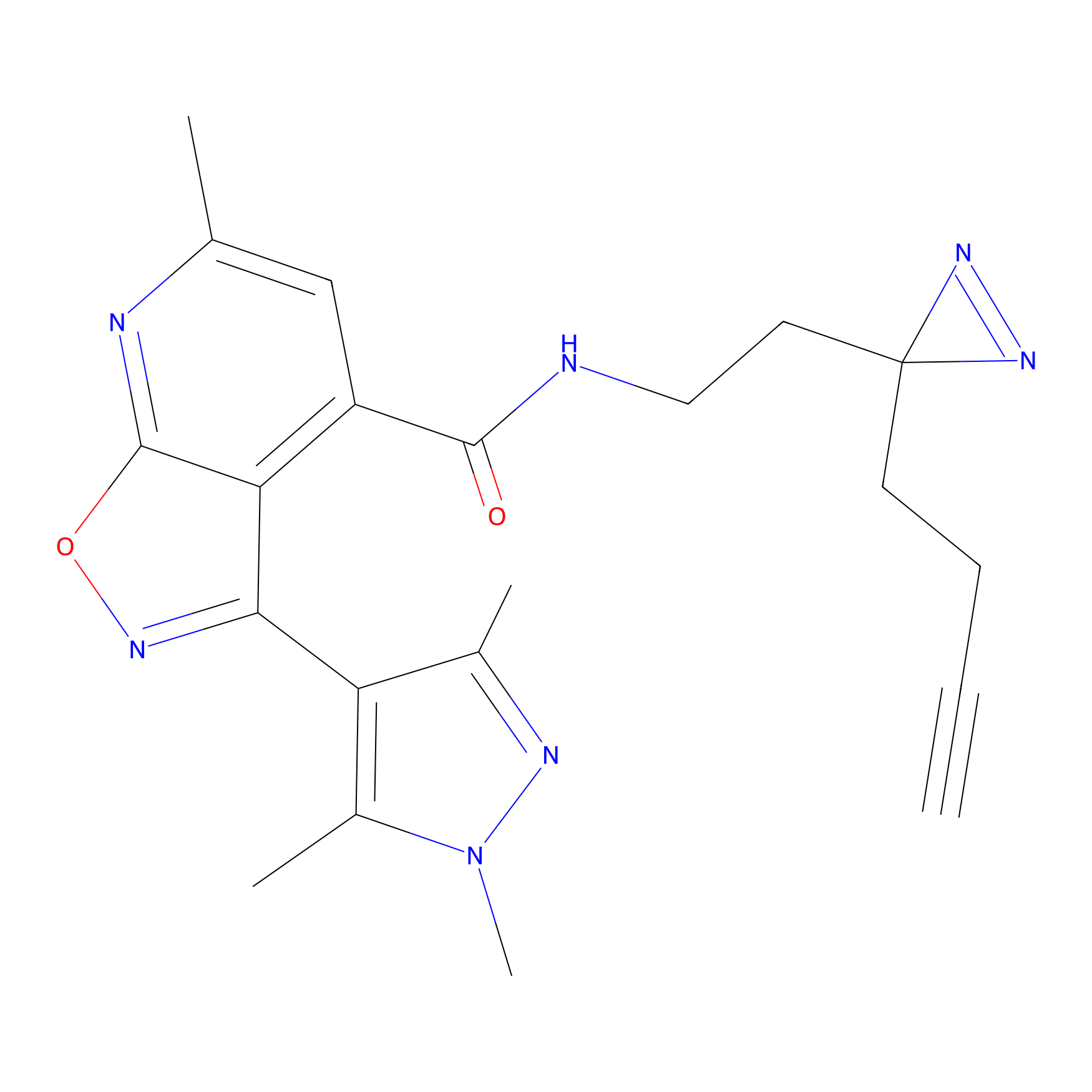
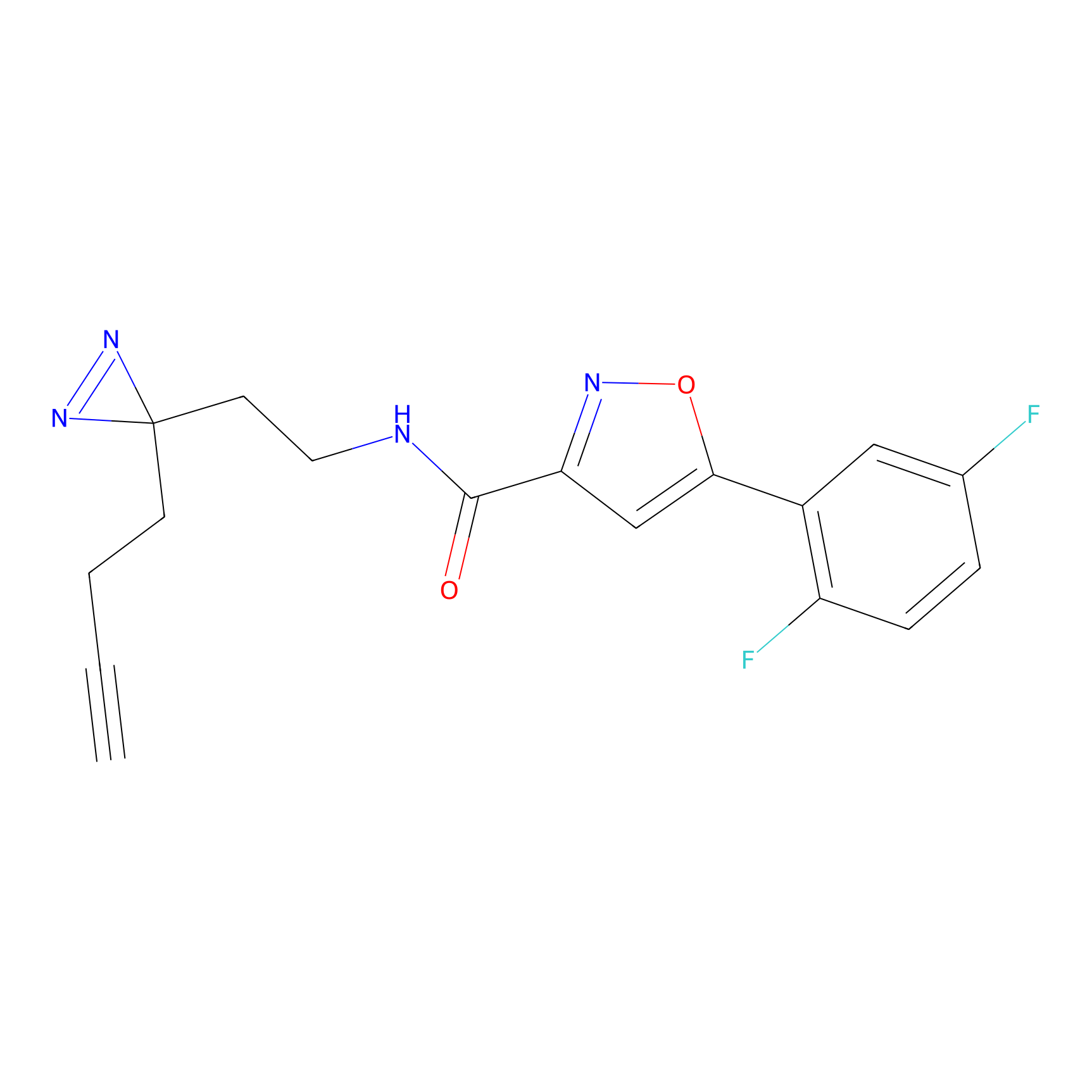
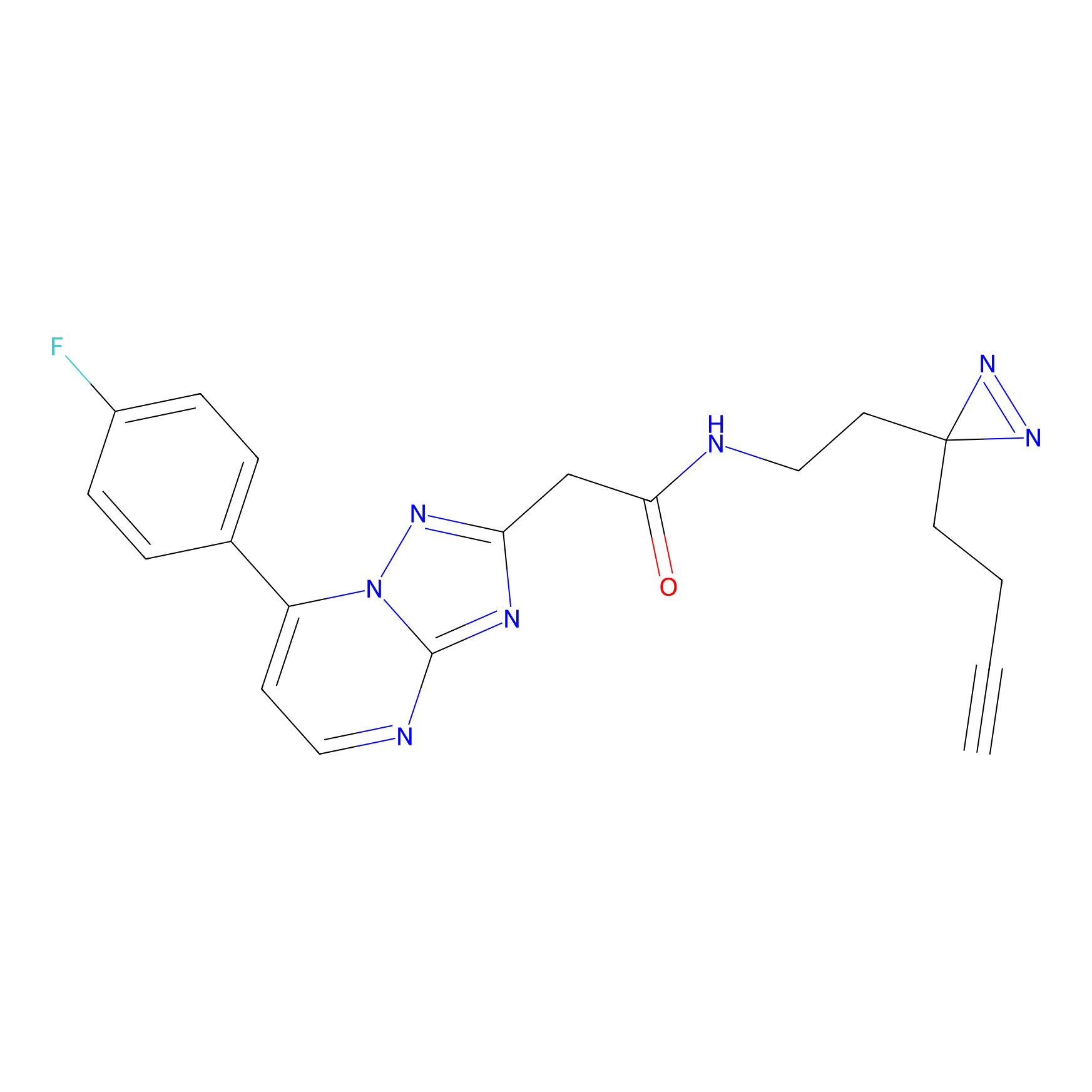
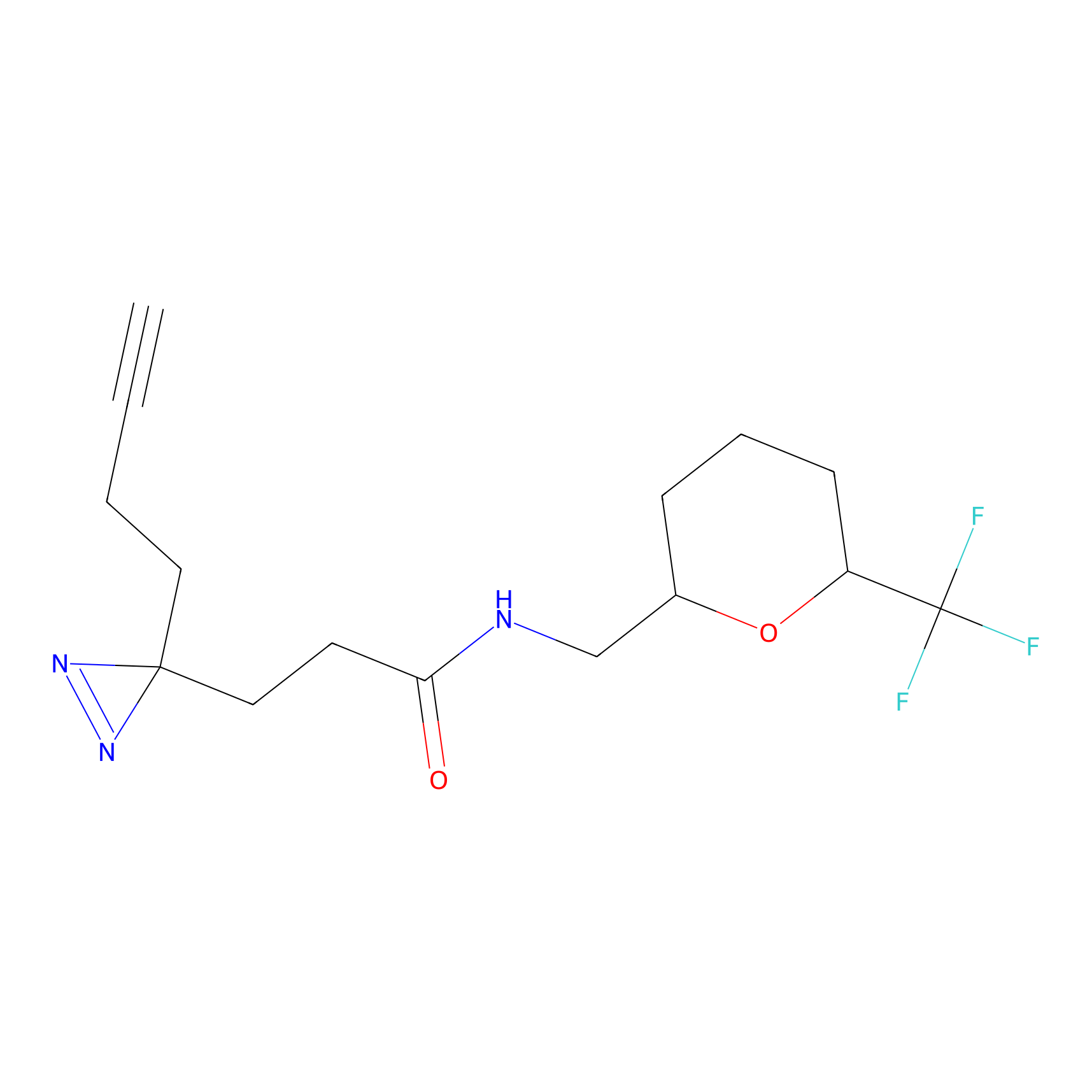
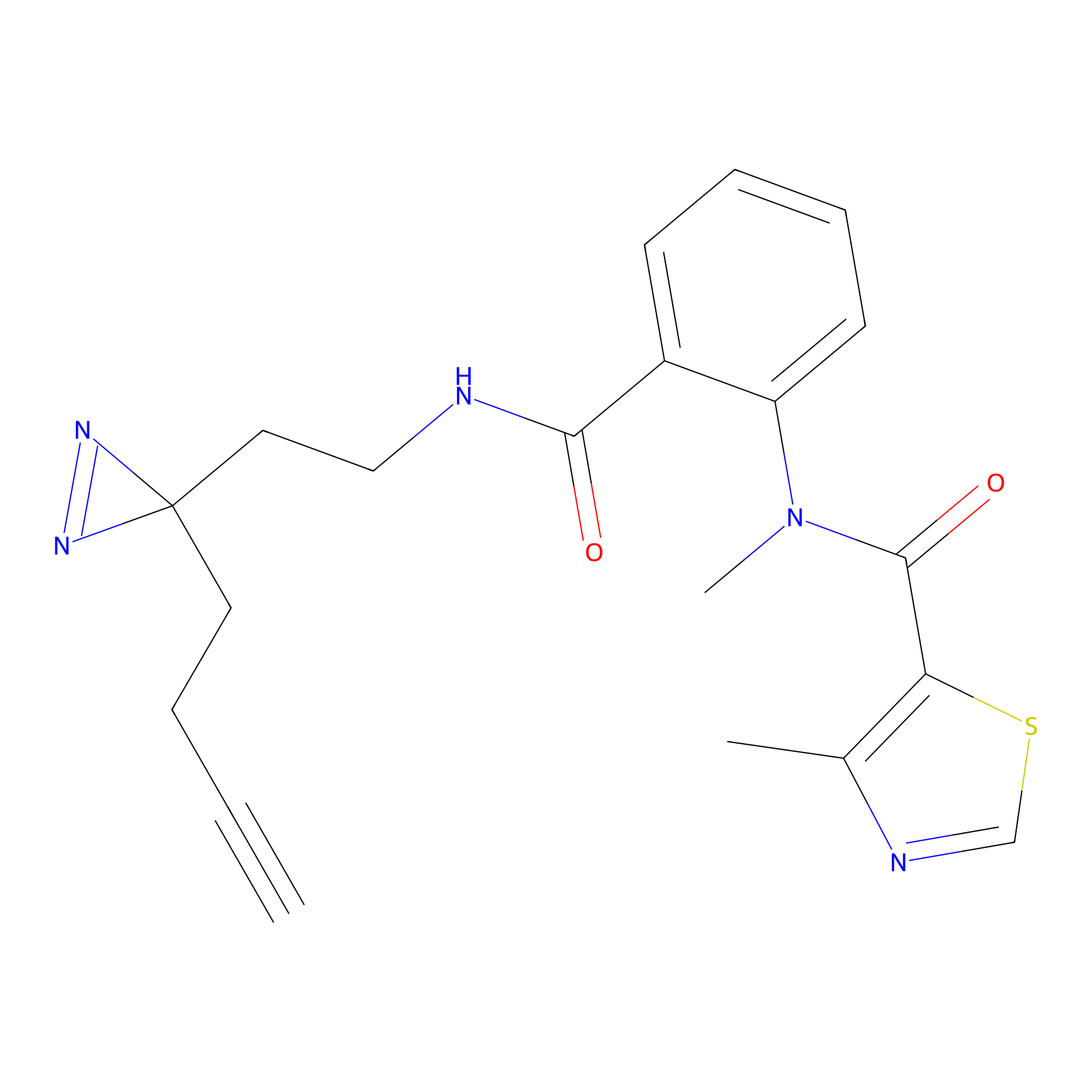
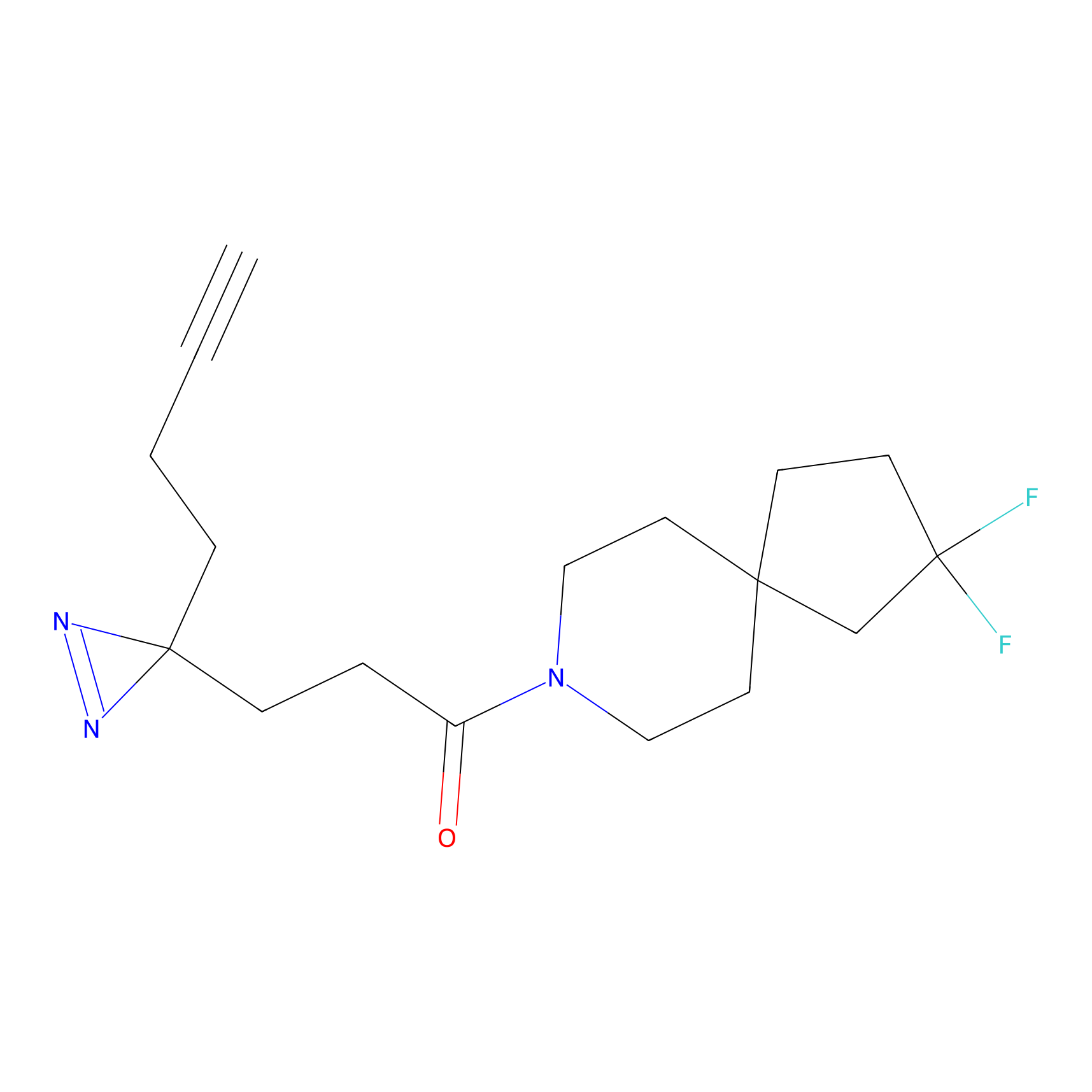
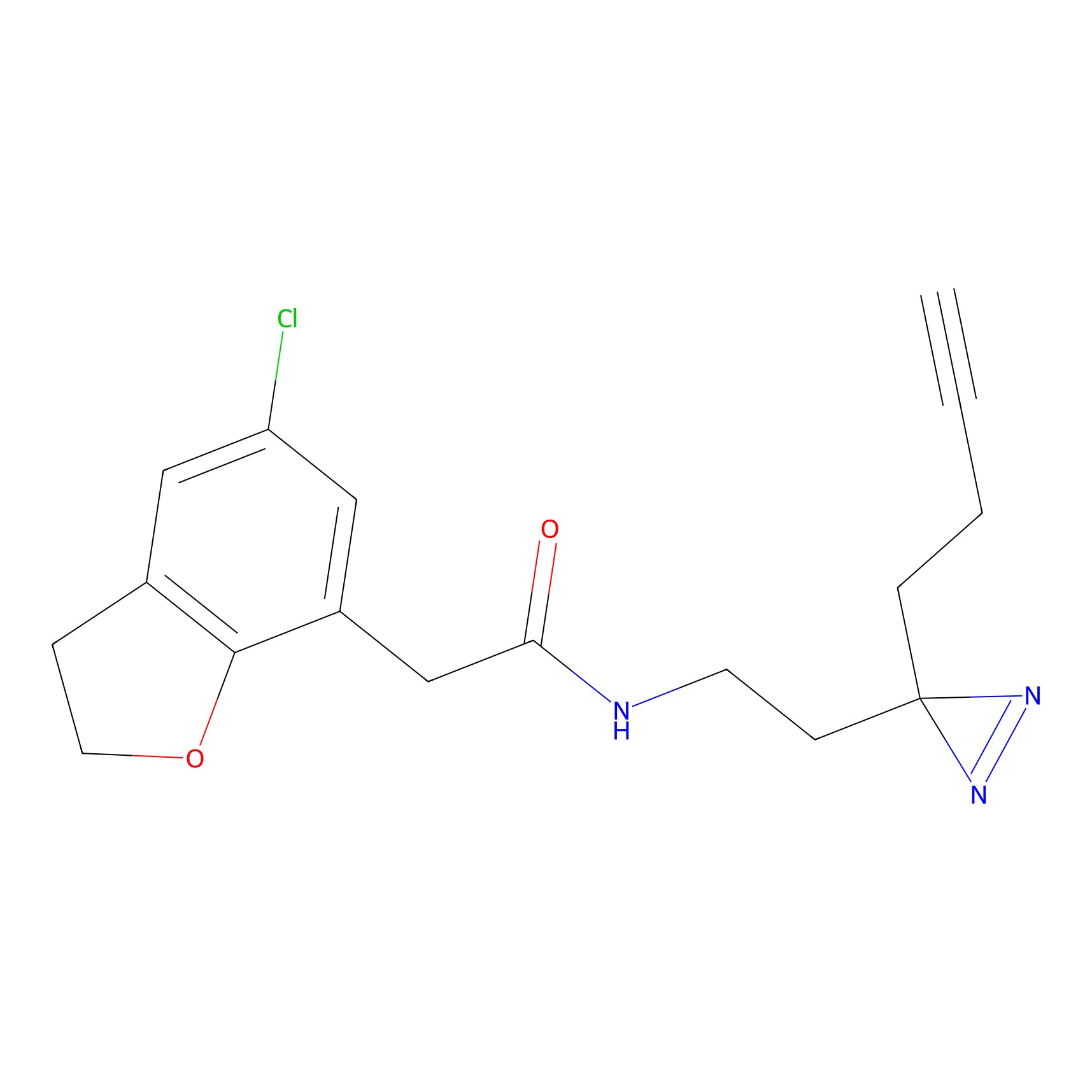
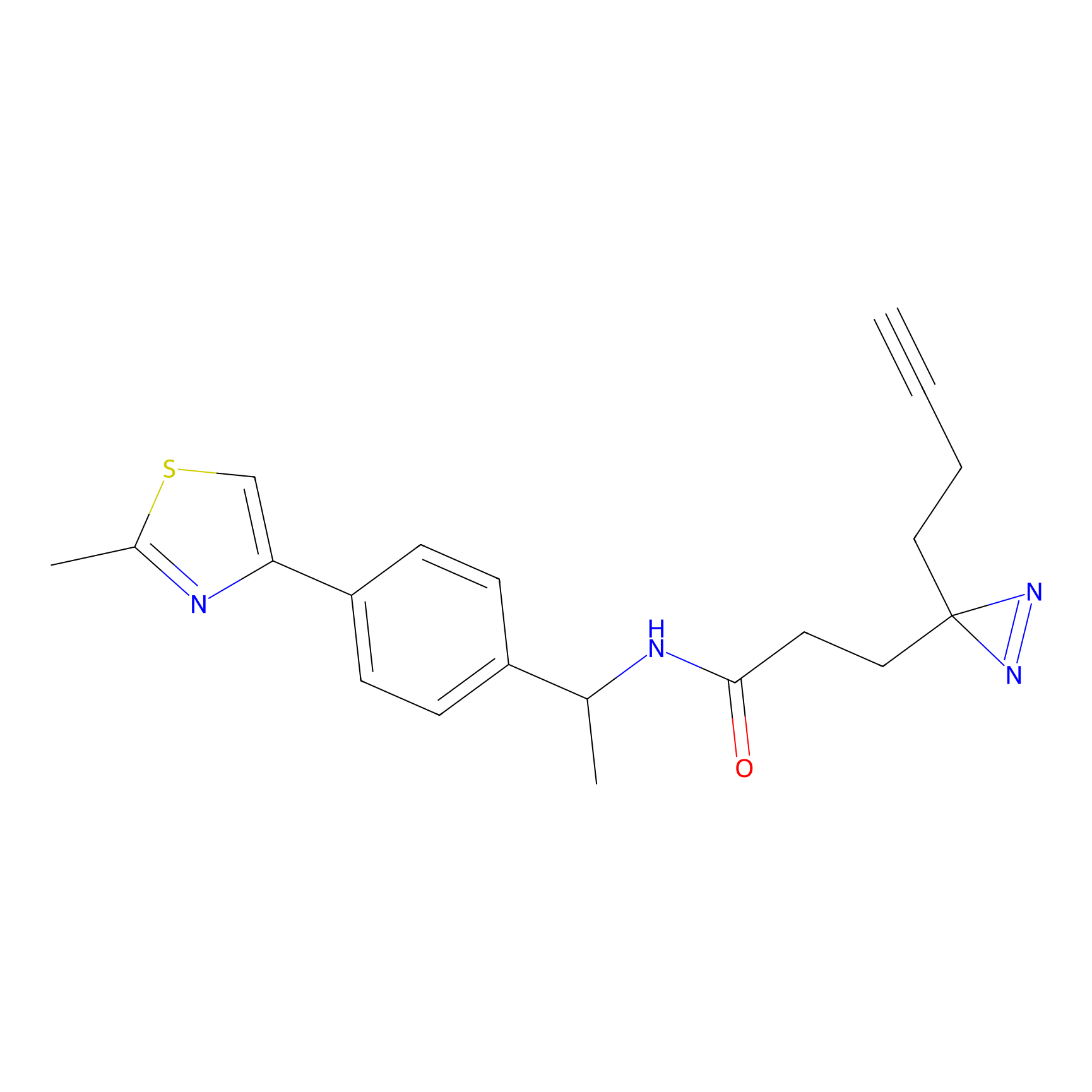
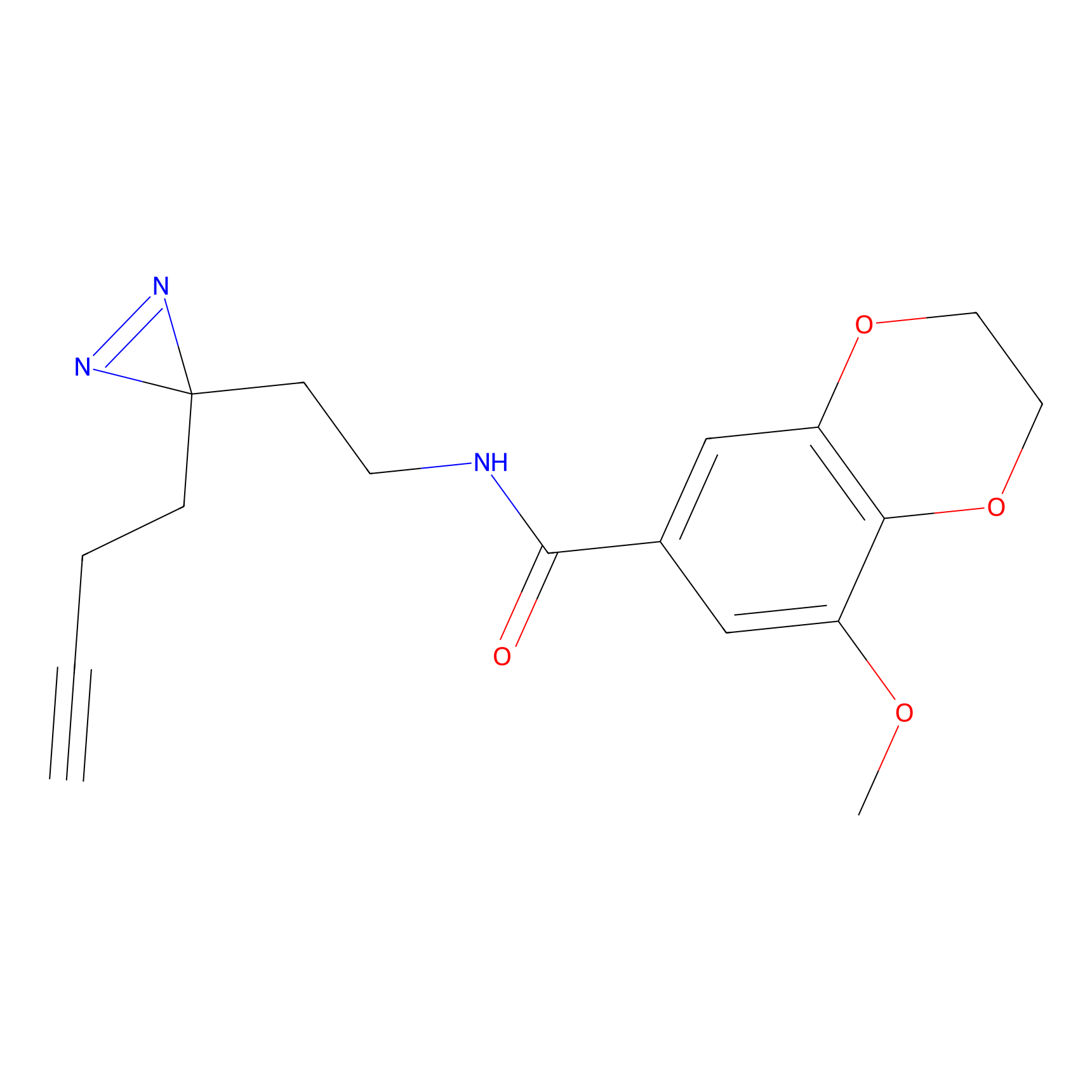
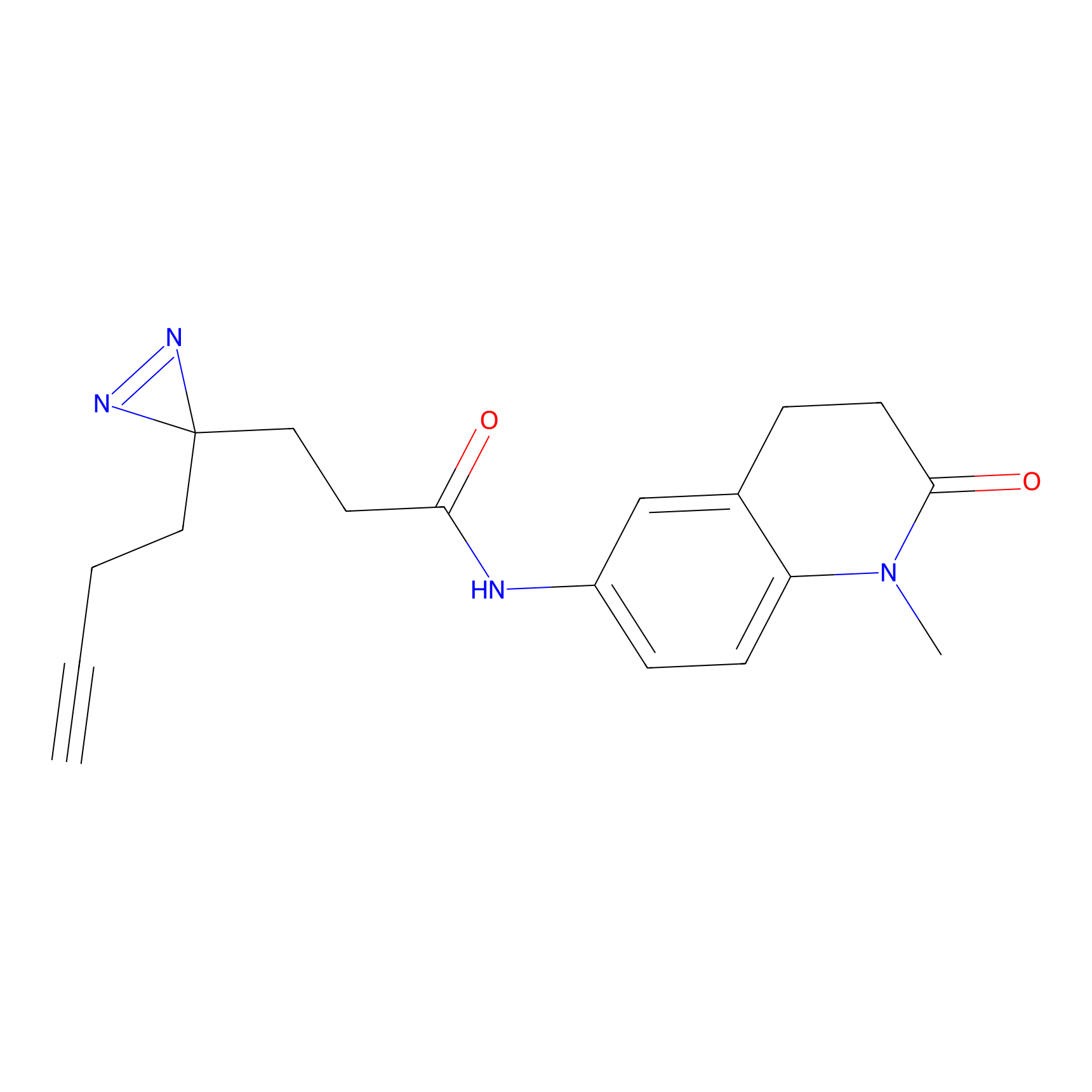
|
YN-1 Probe Info |
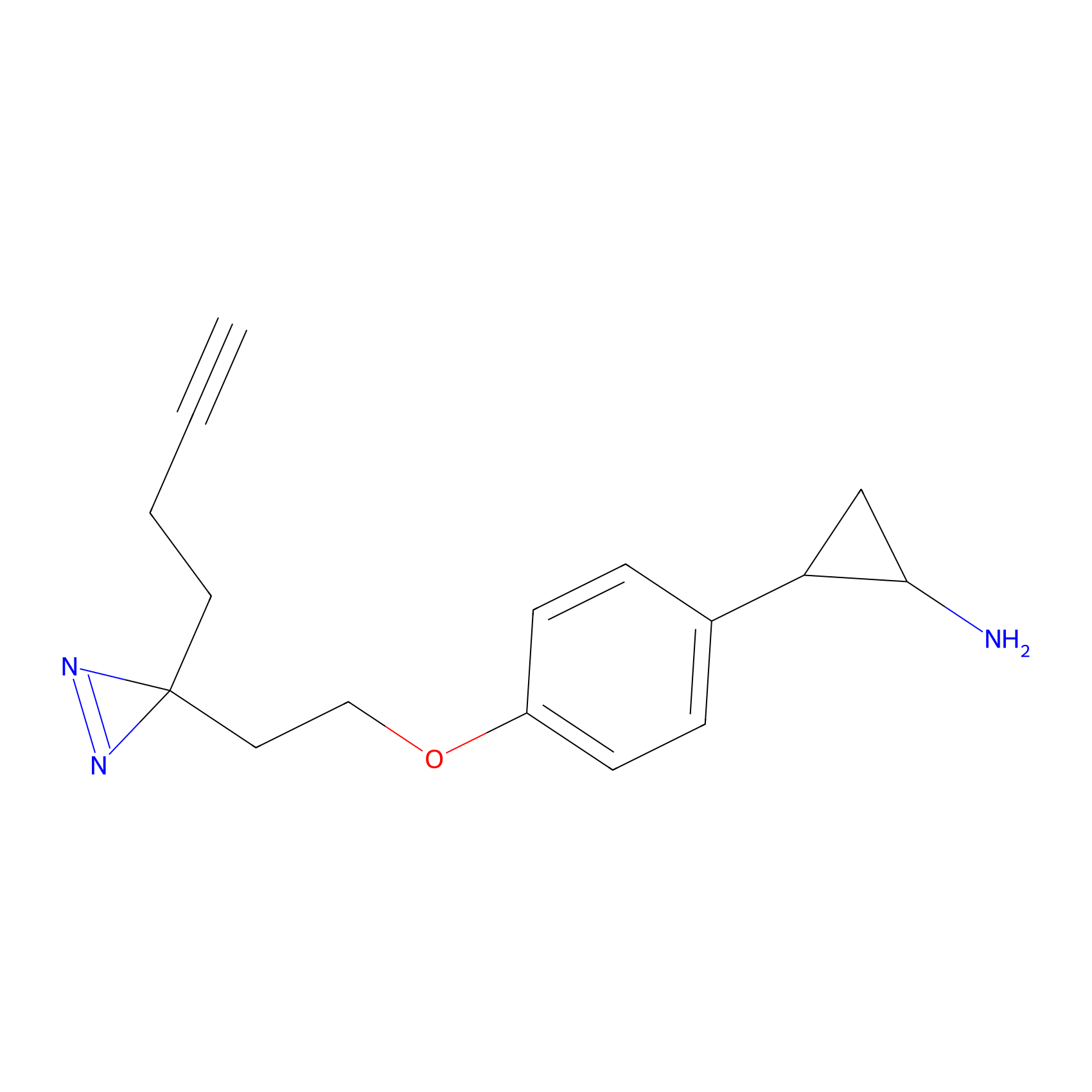
 |
100.00 | LDD0444 | [2] | |
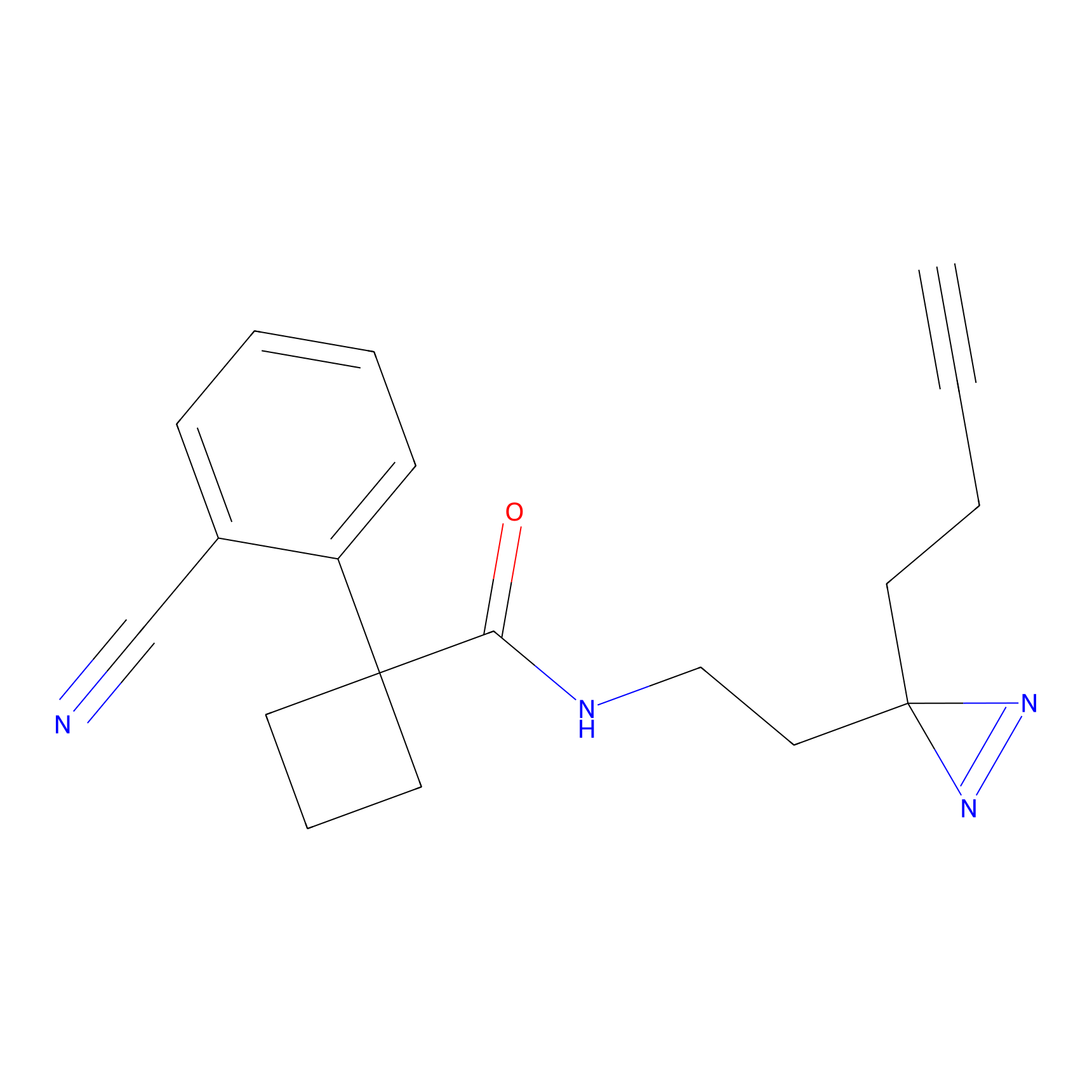
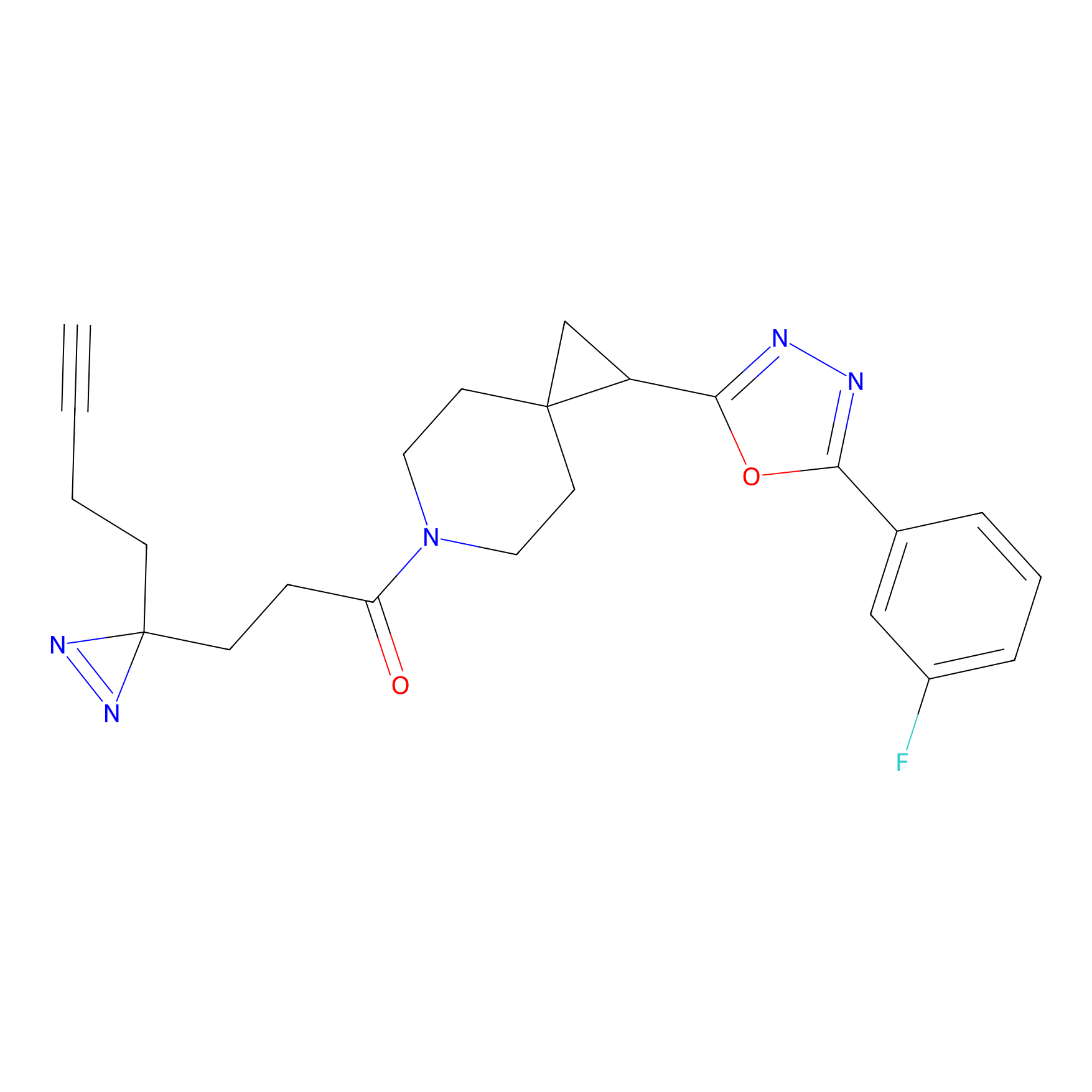
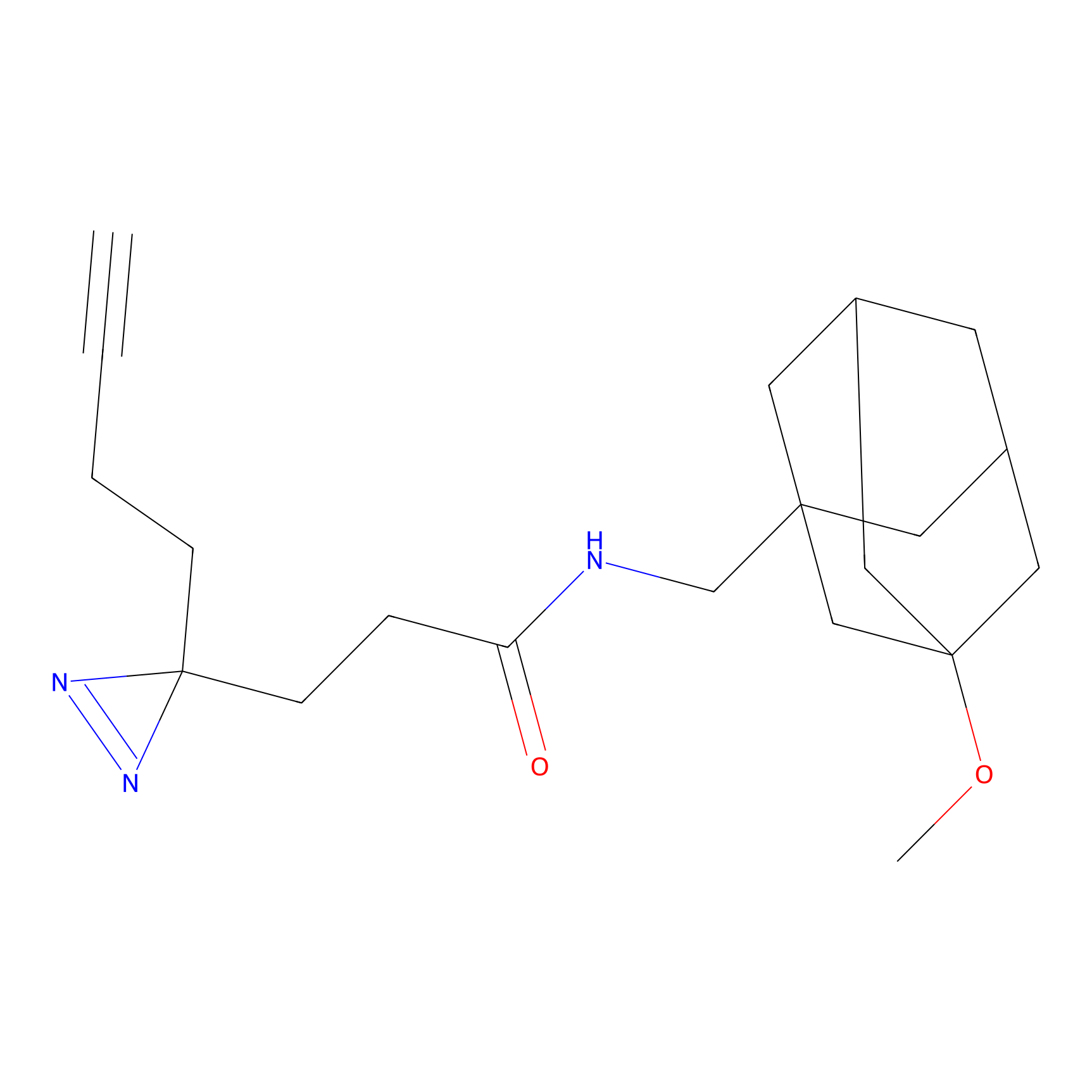
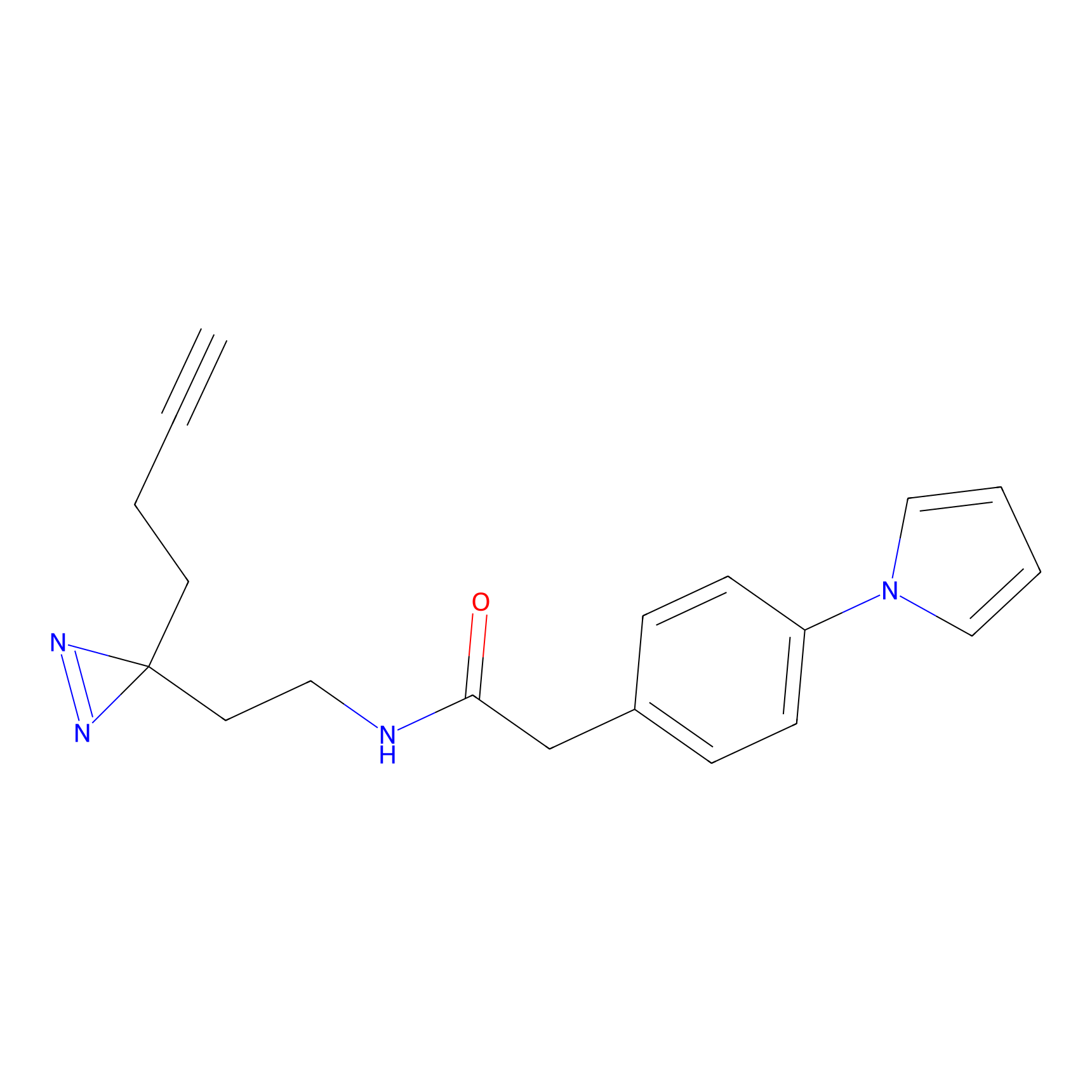
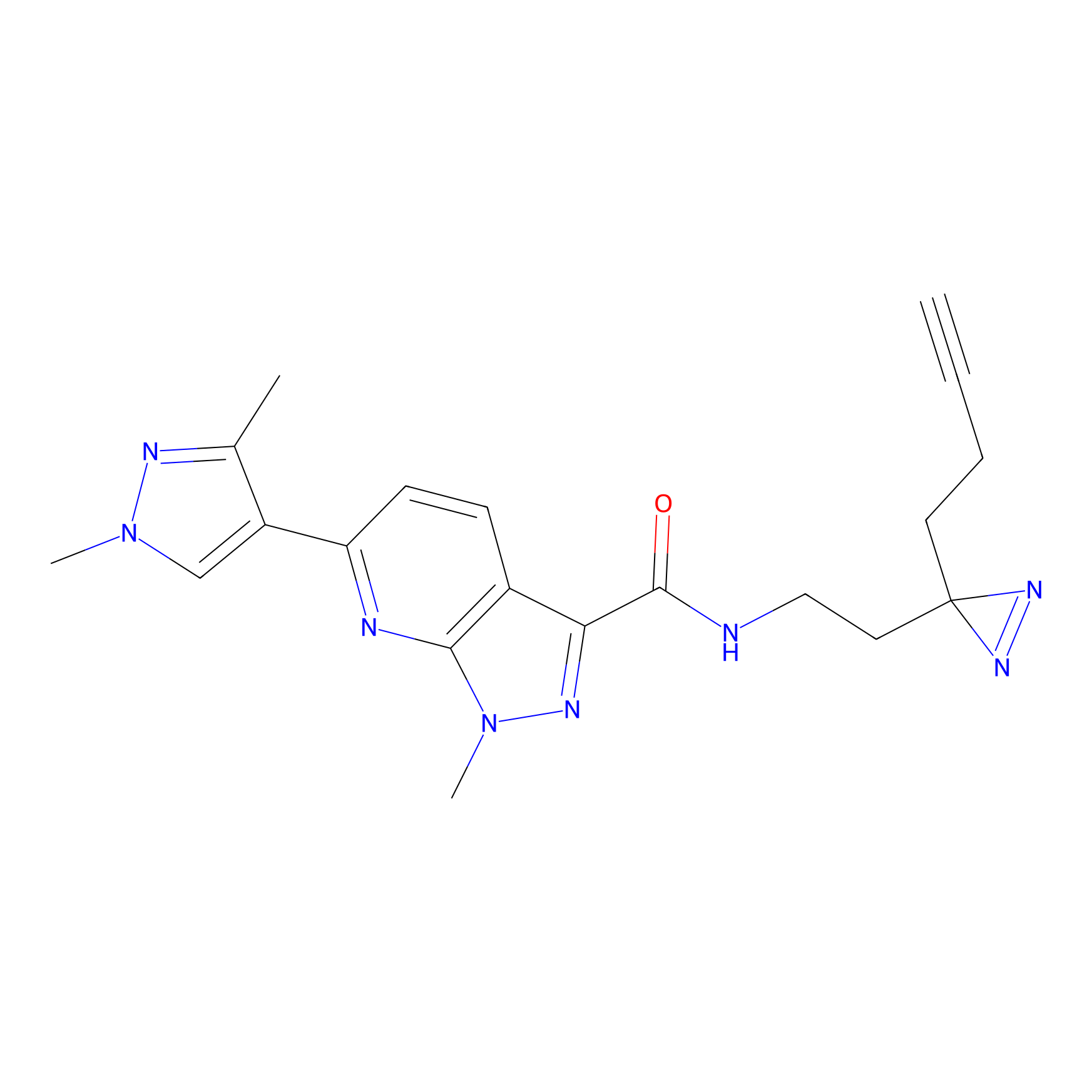
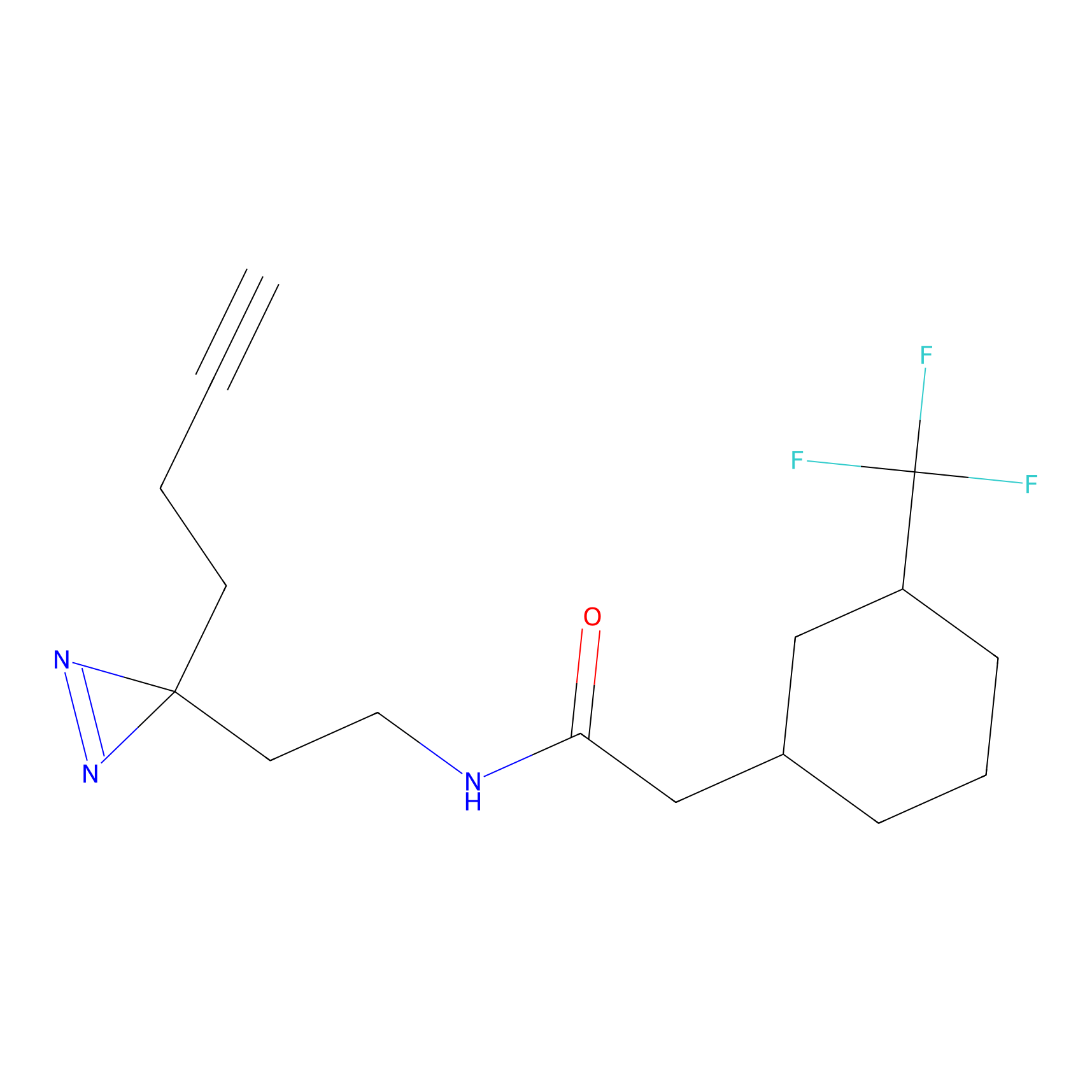
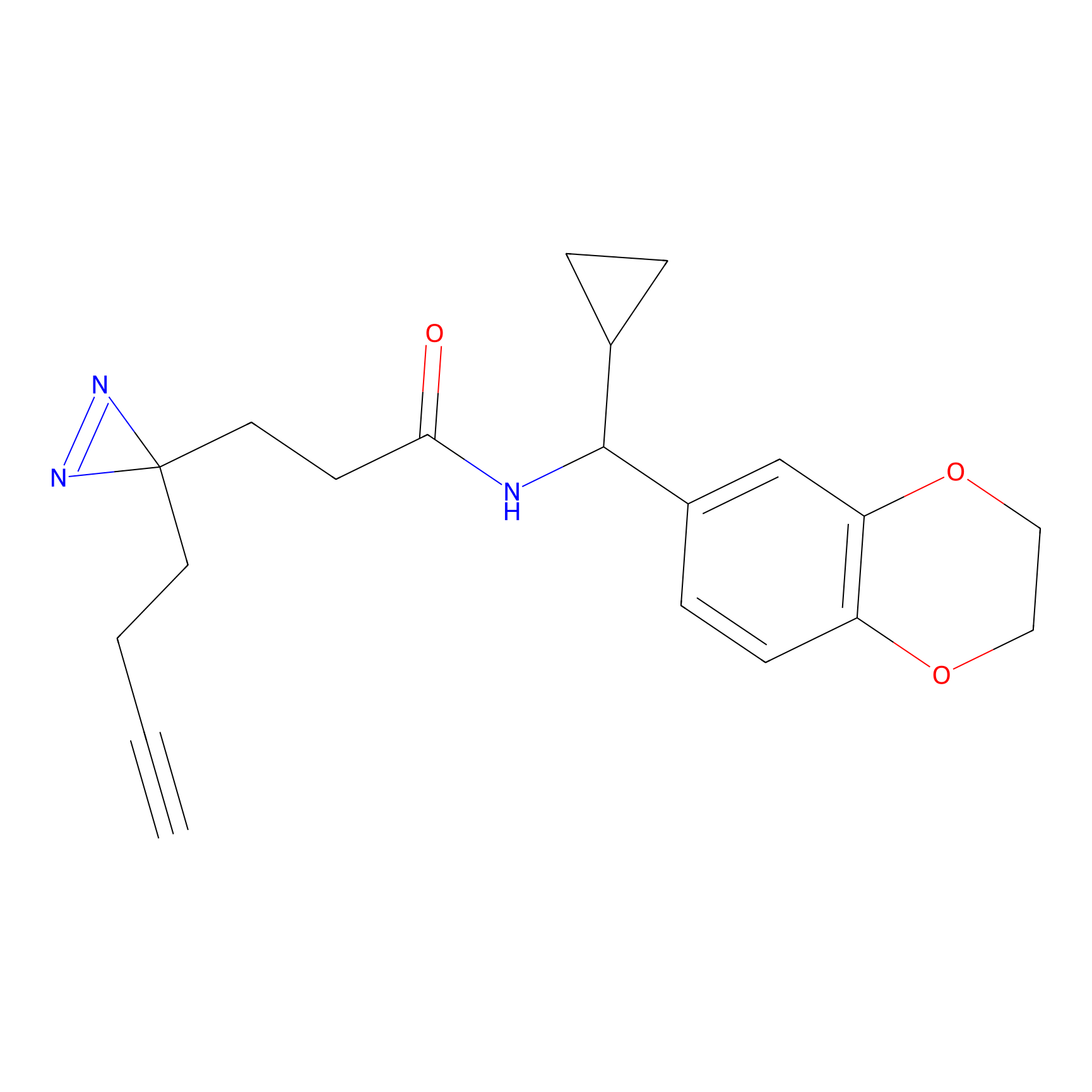
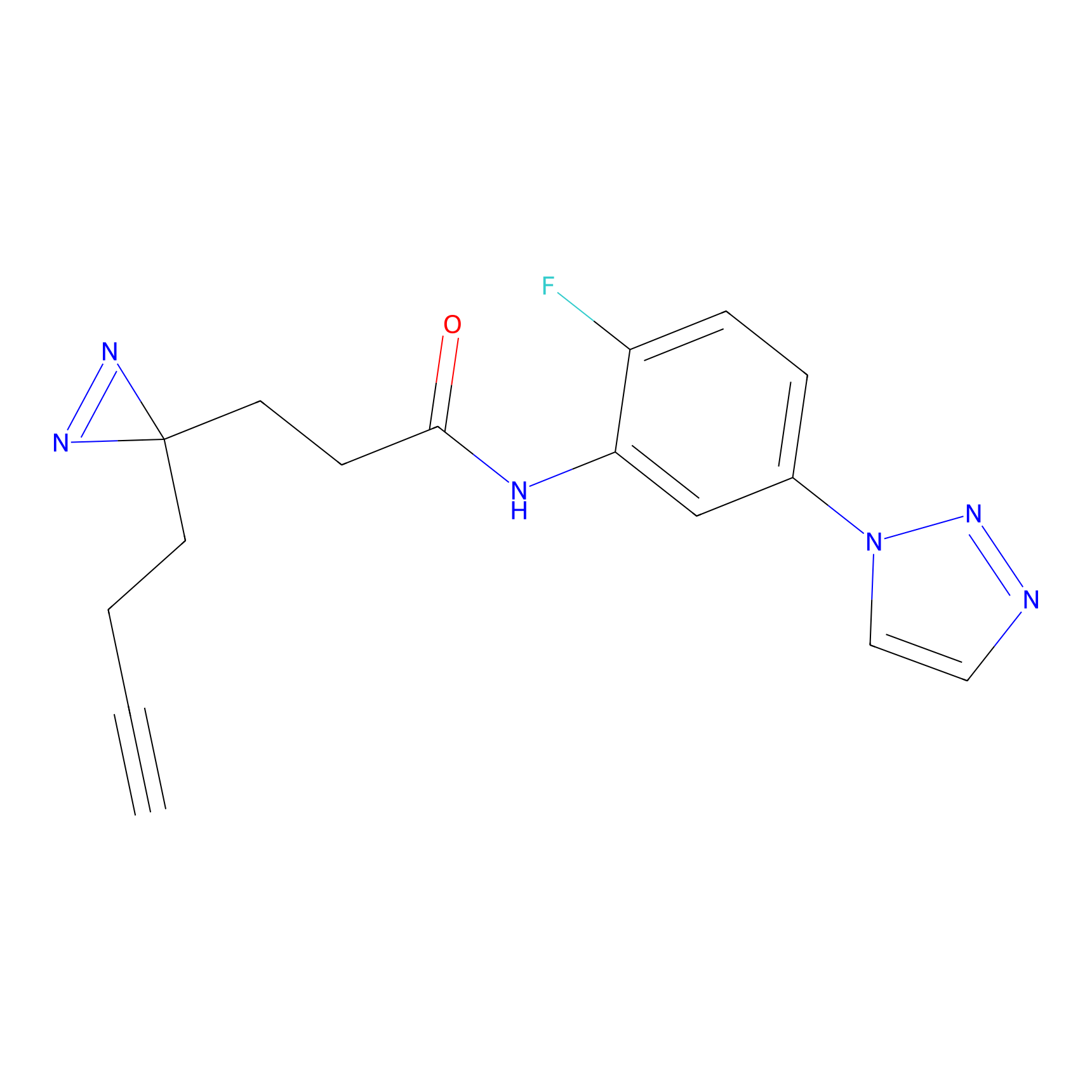
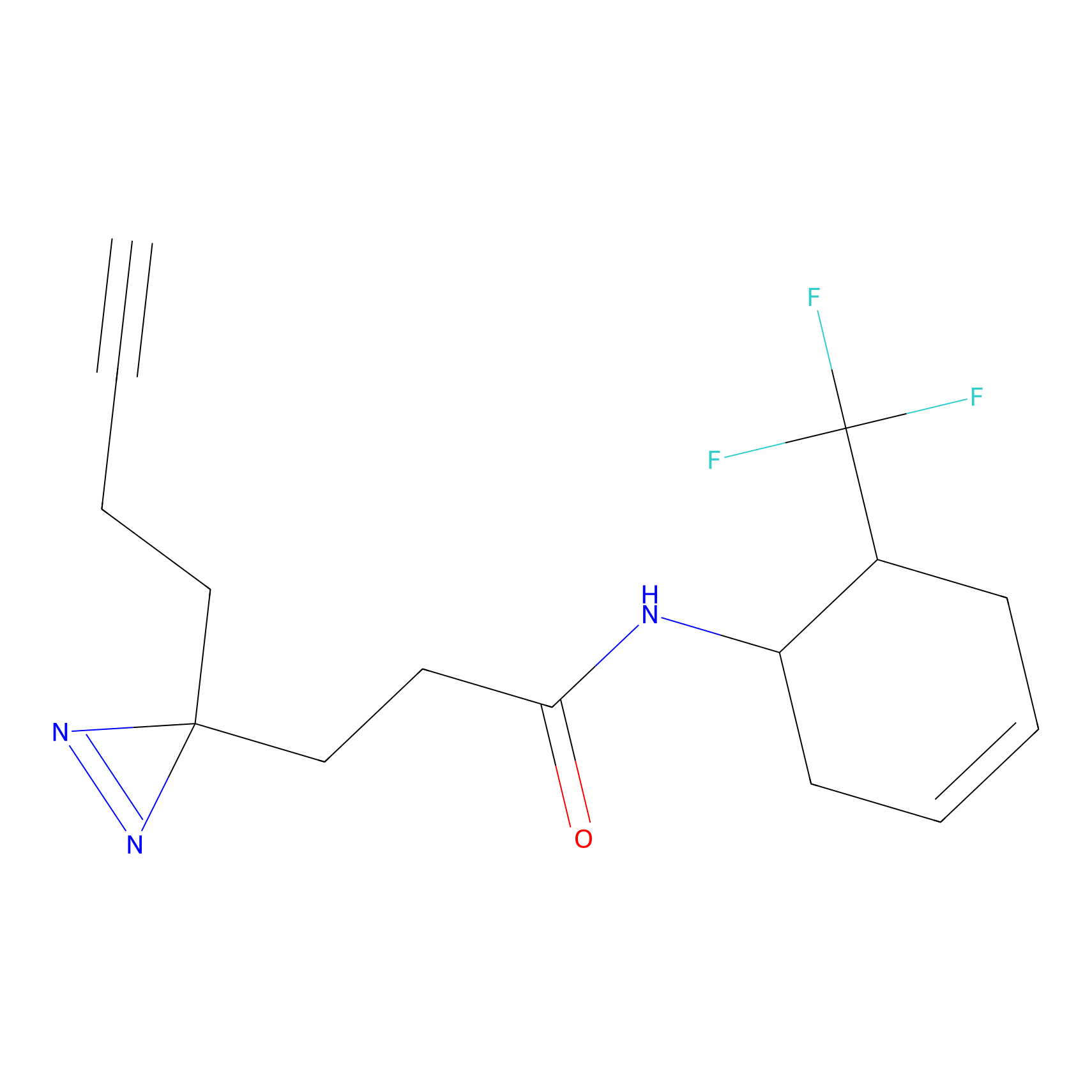
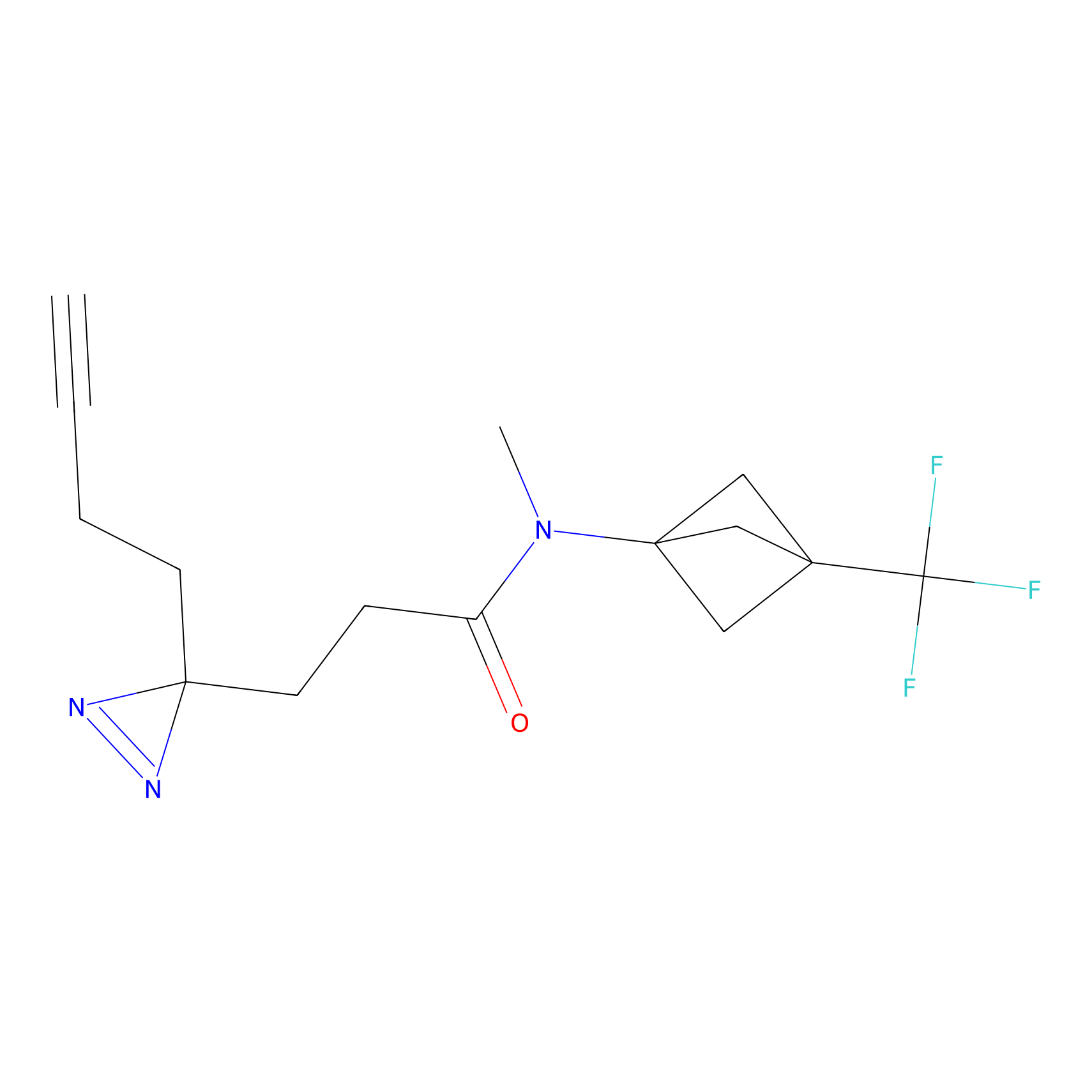
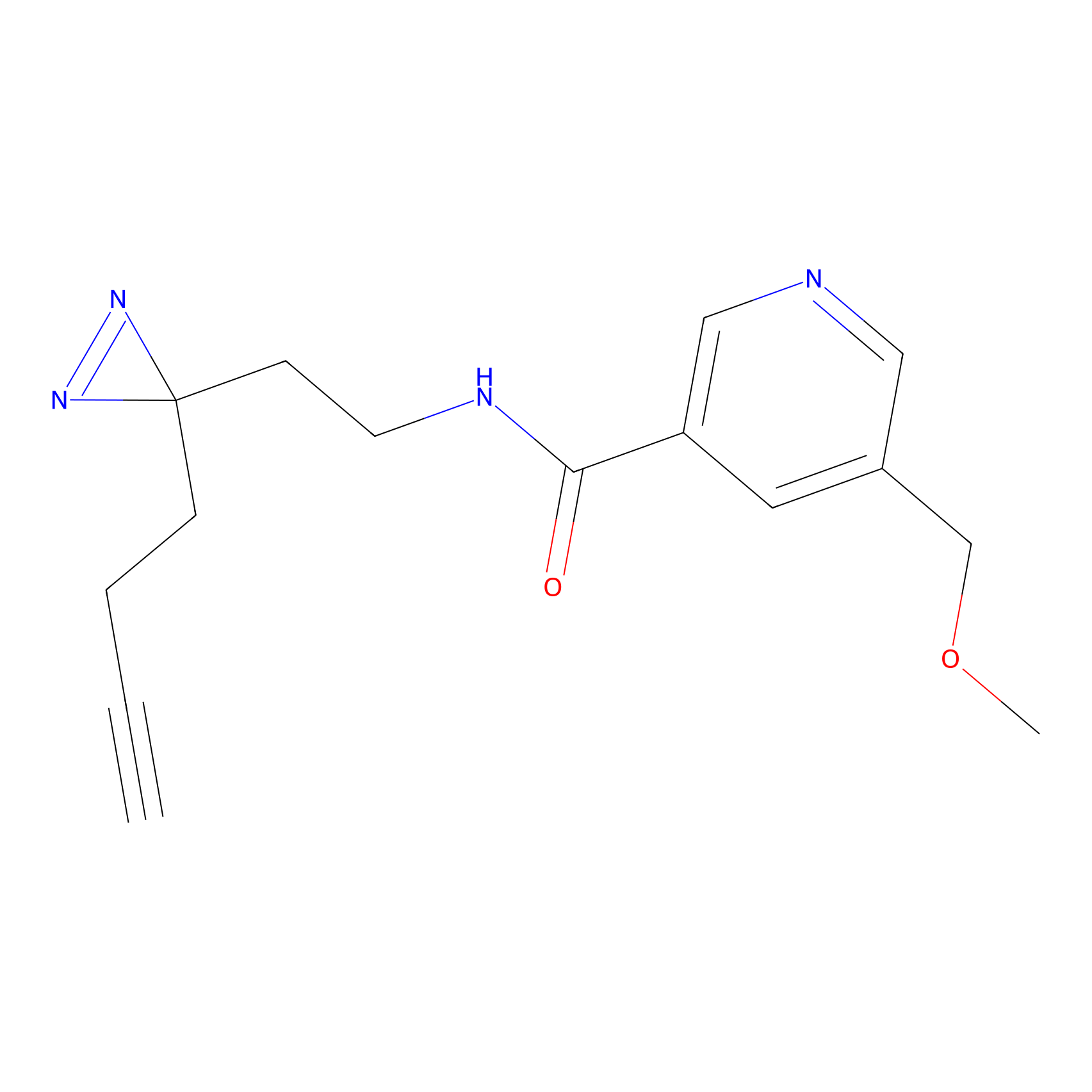
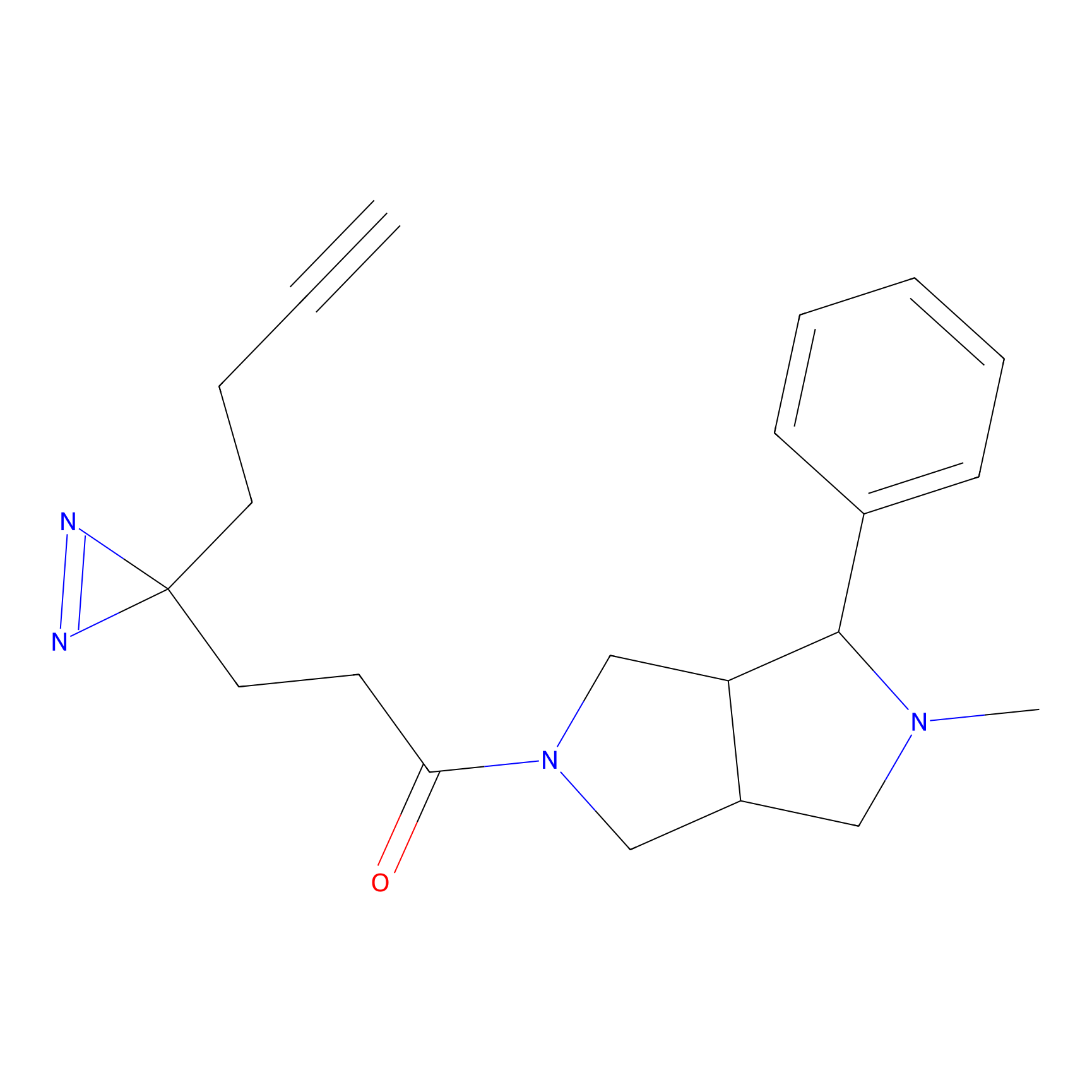
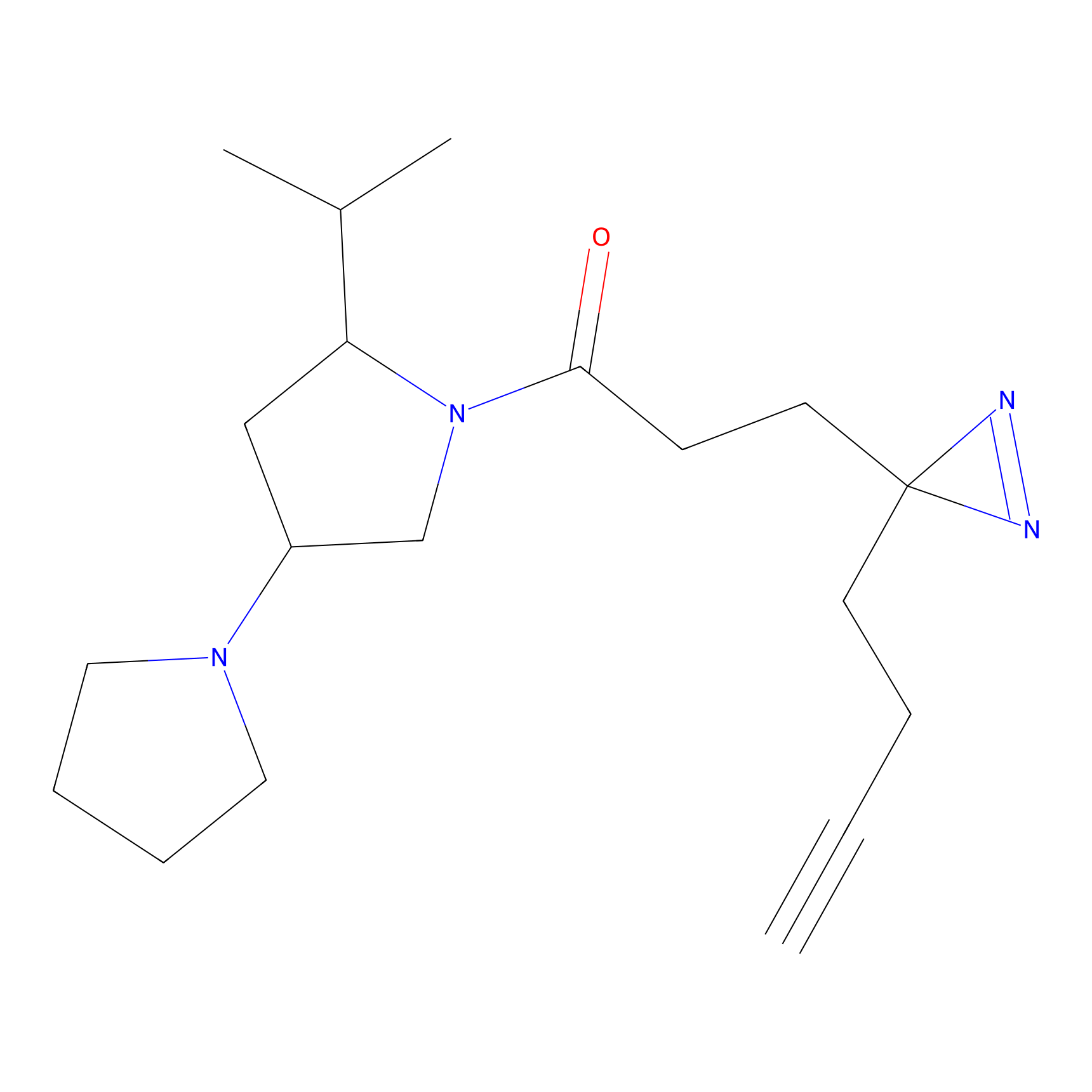
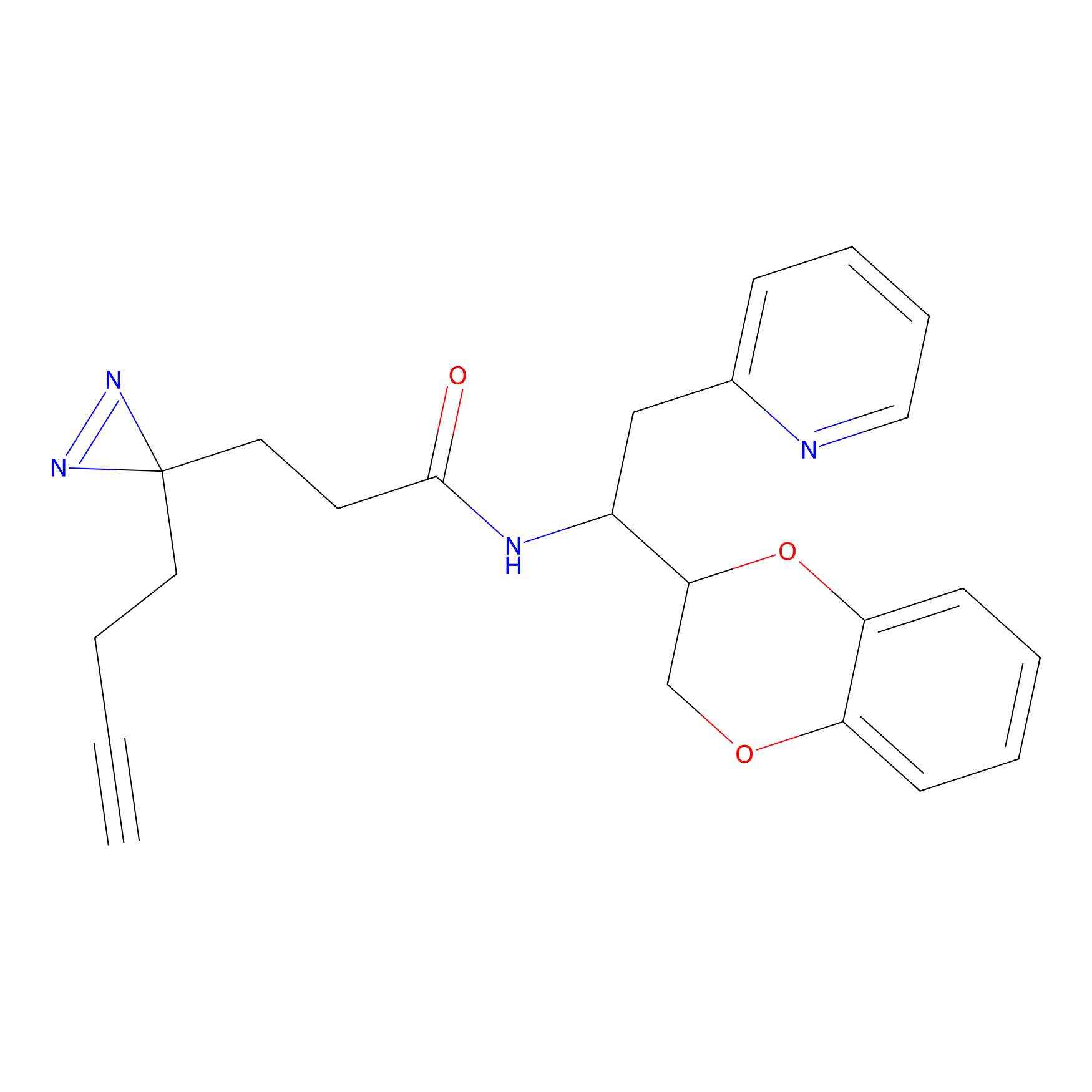
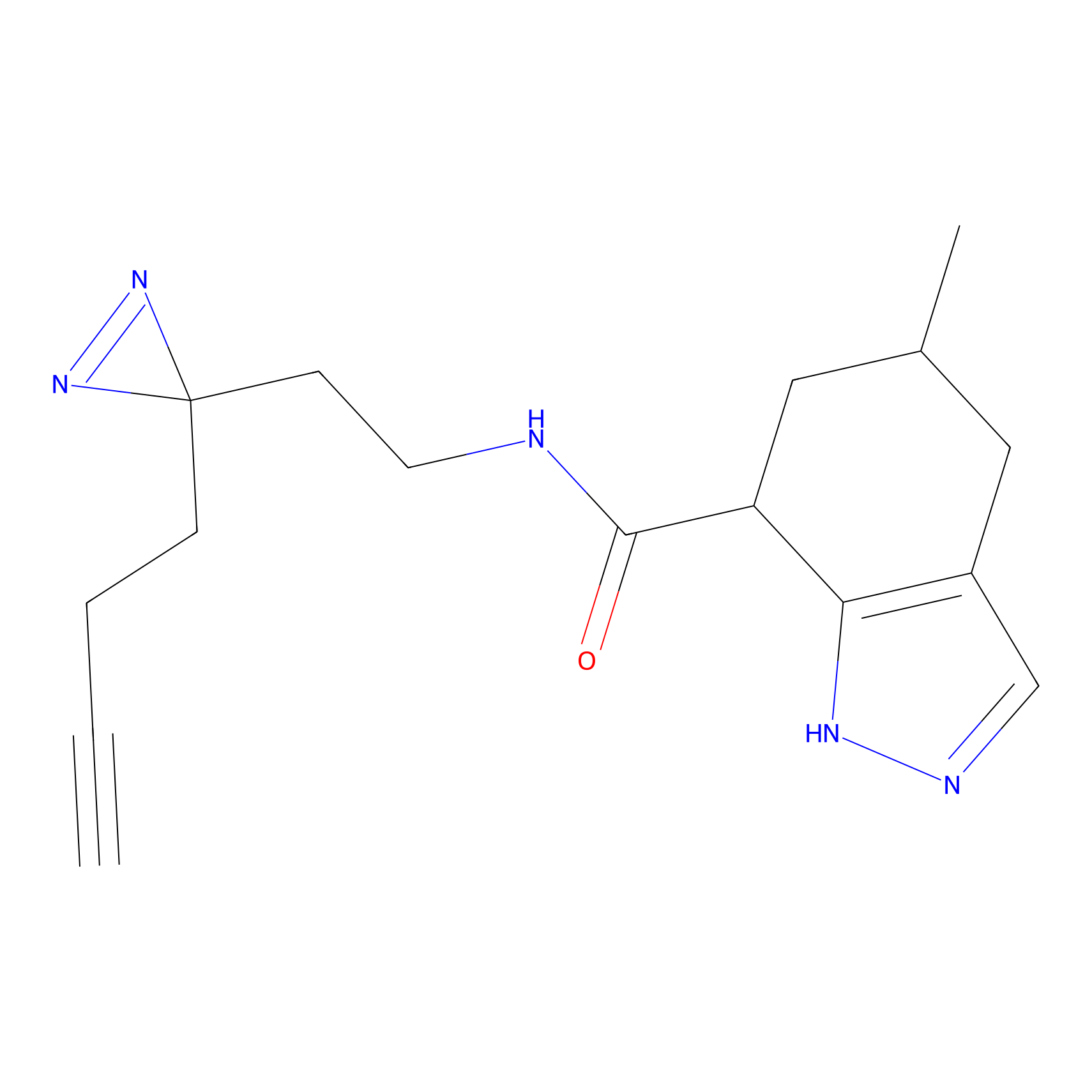
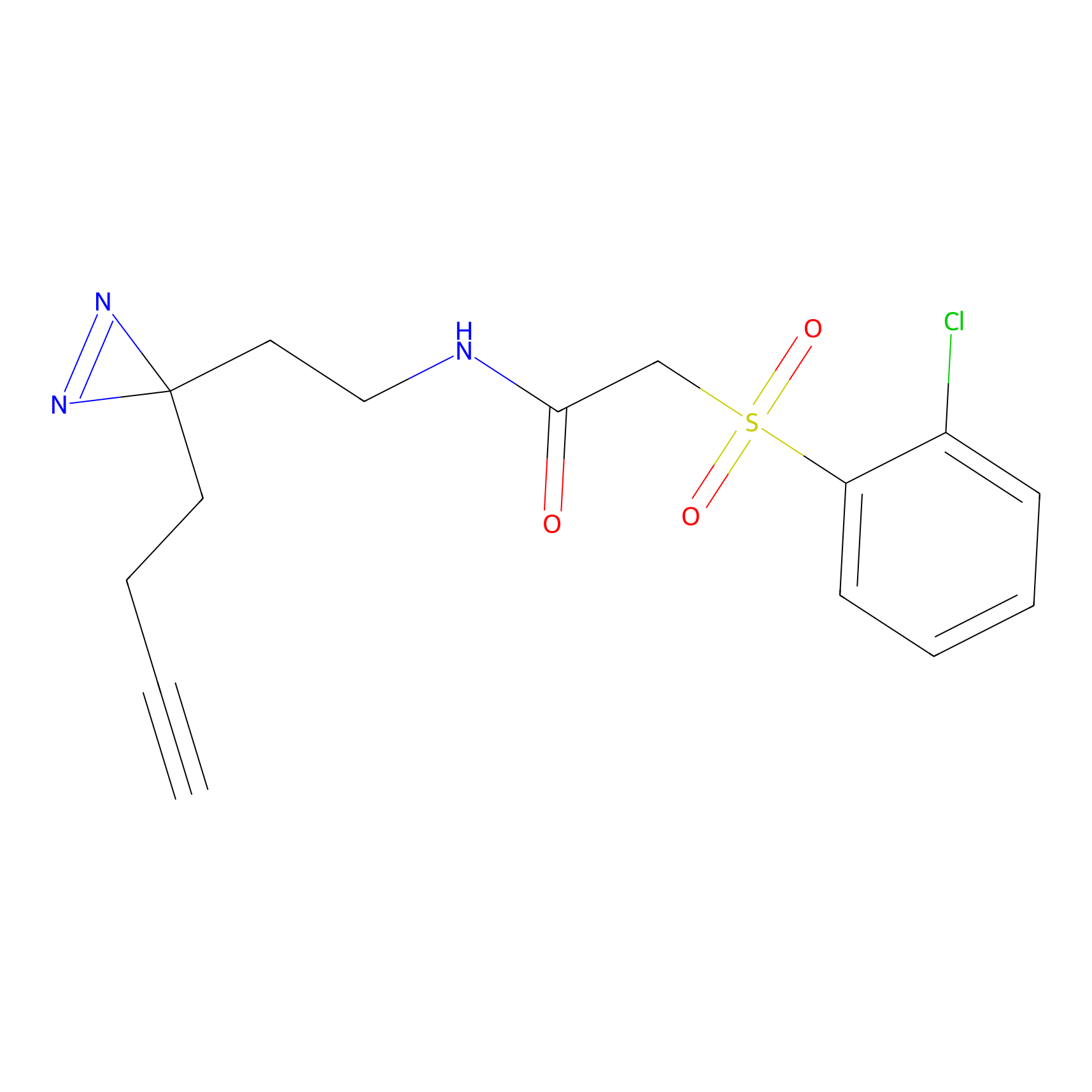
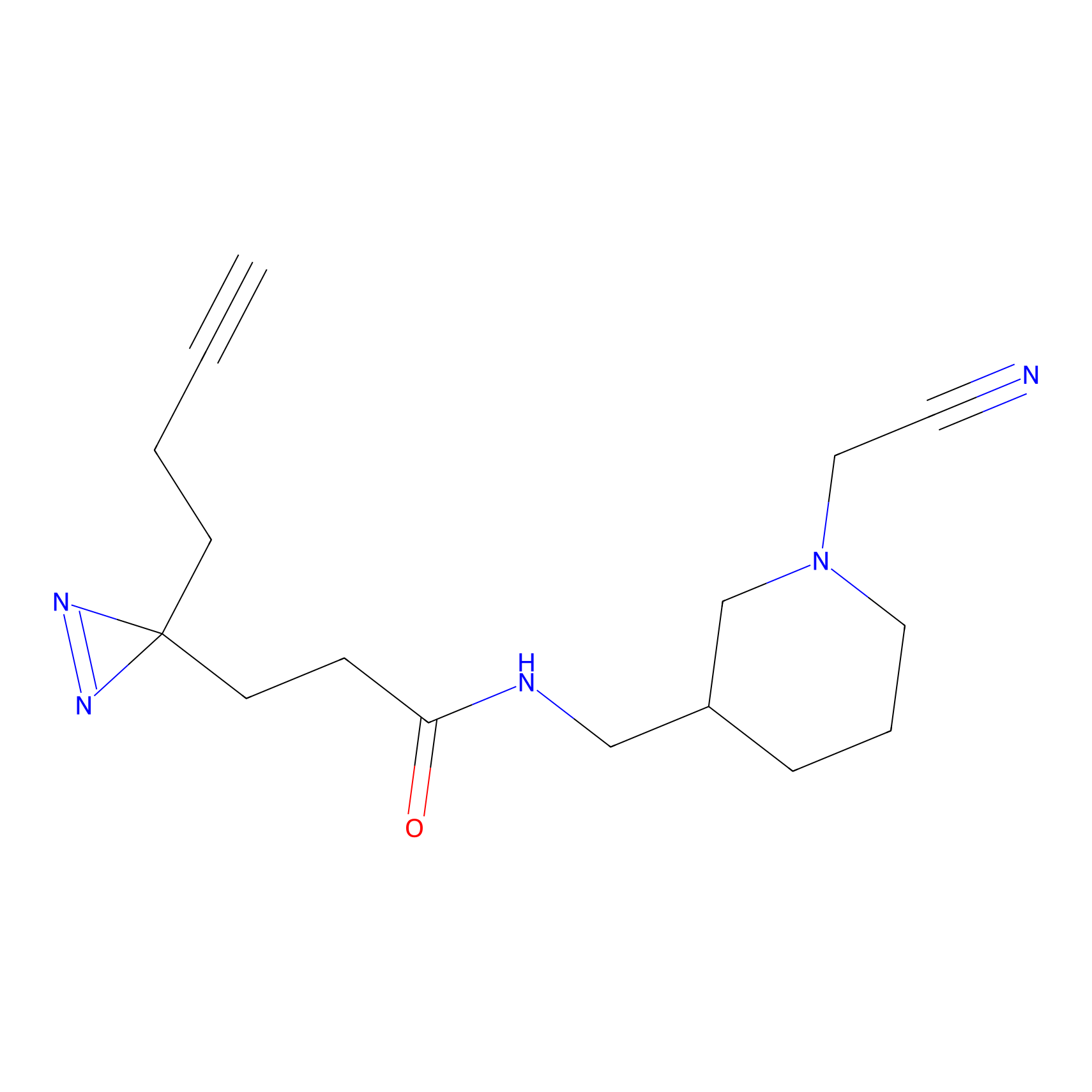
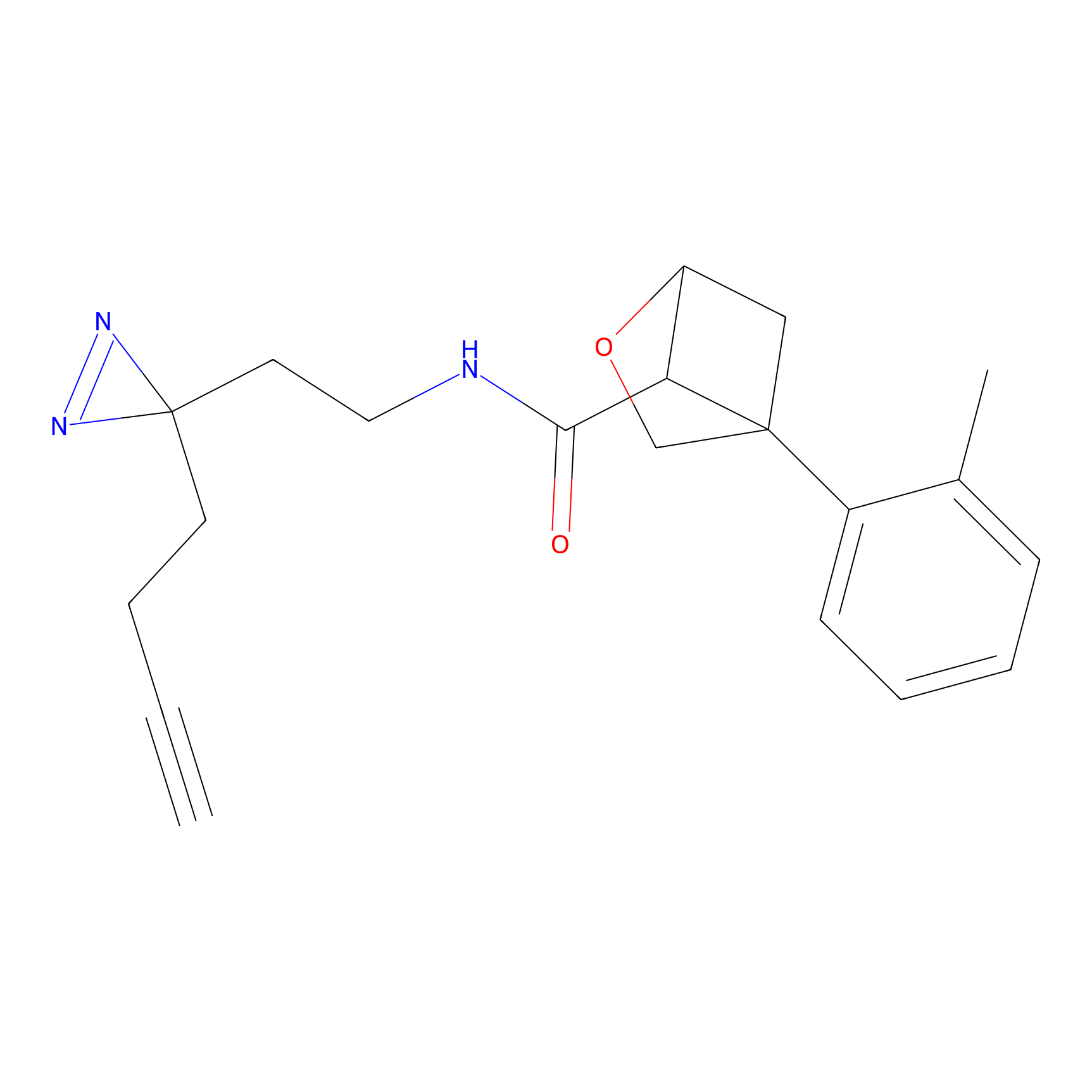
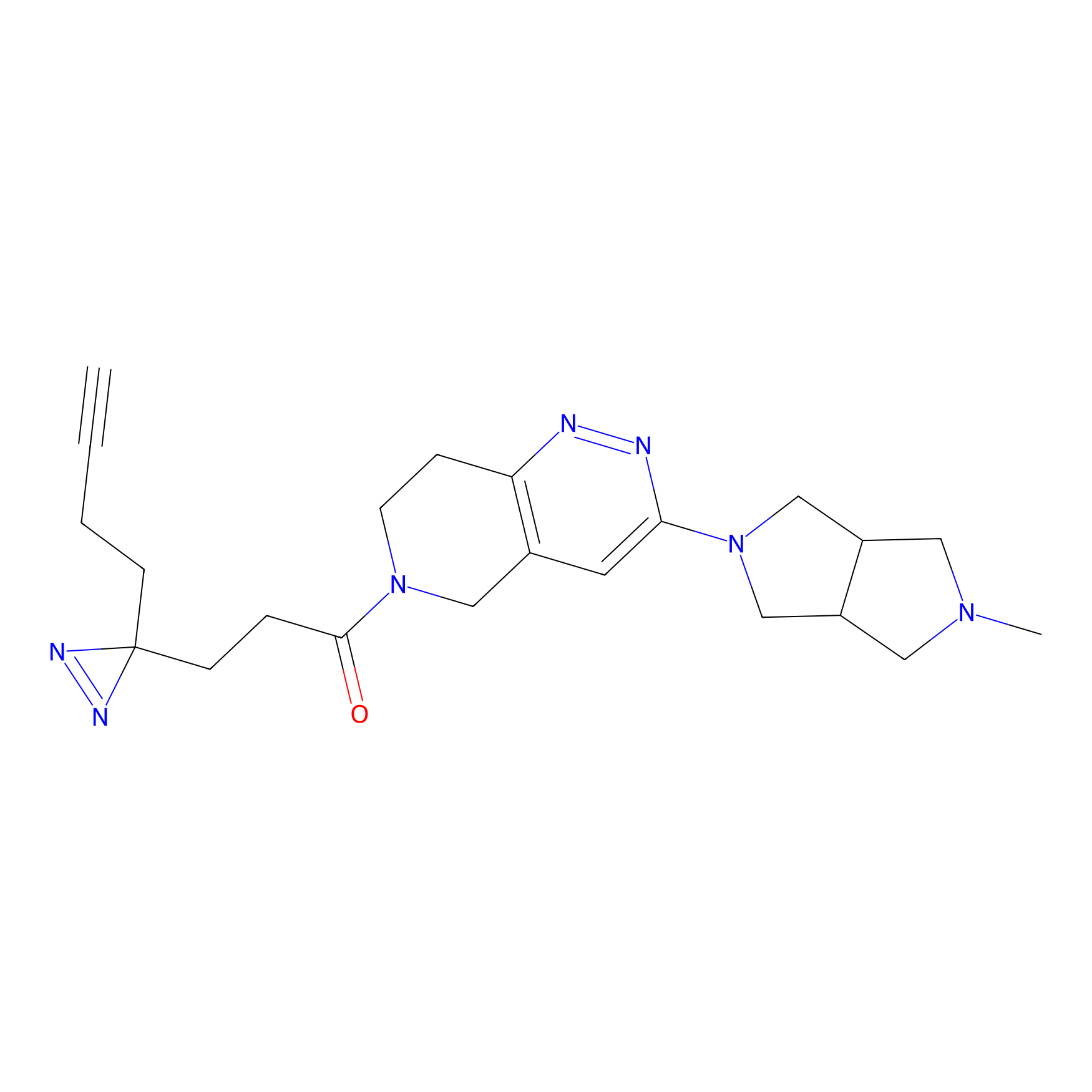
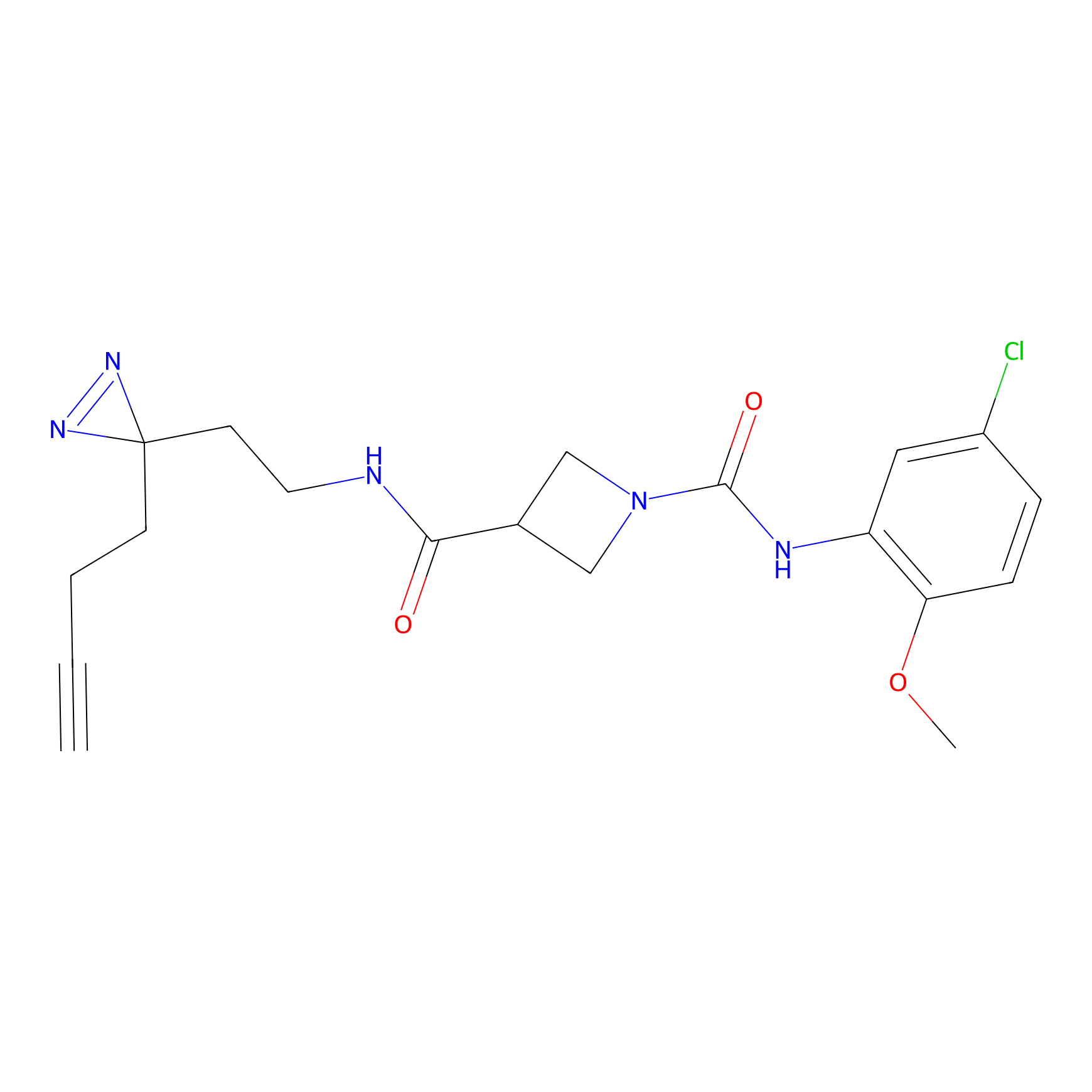
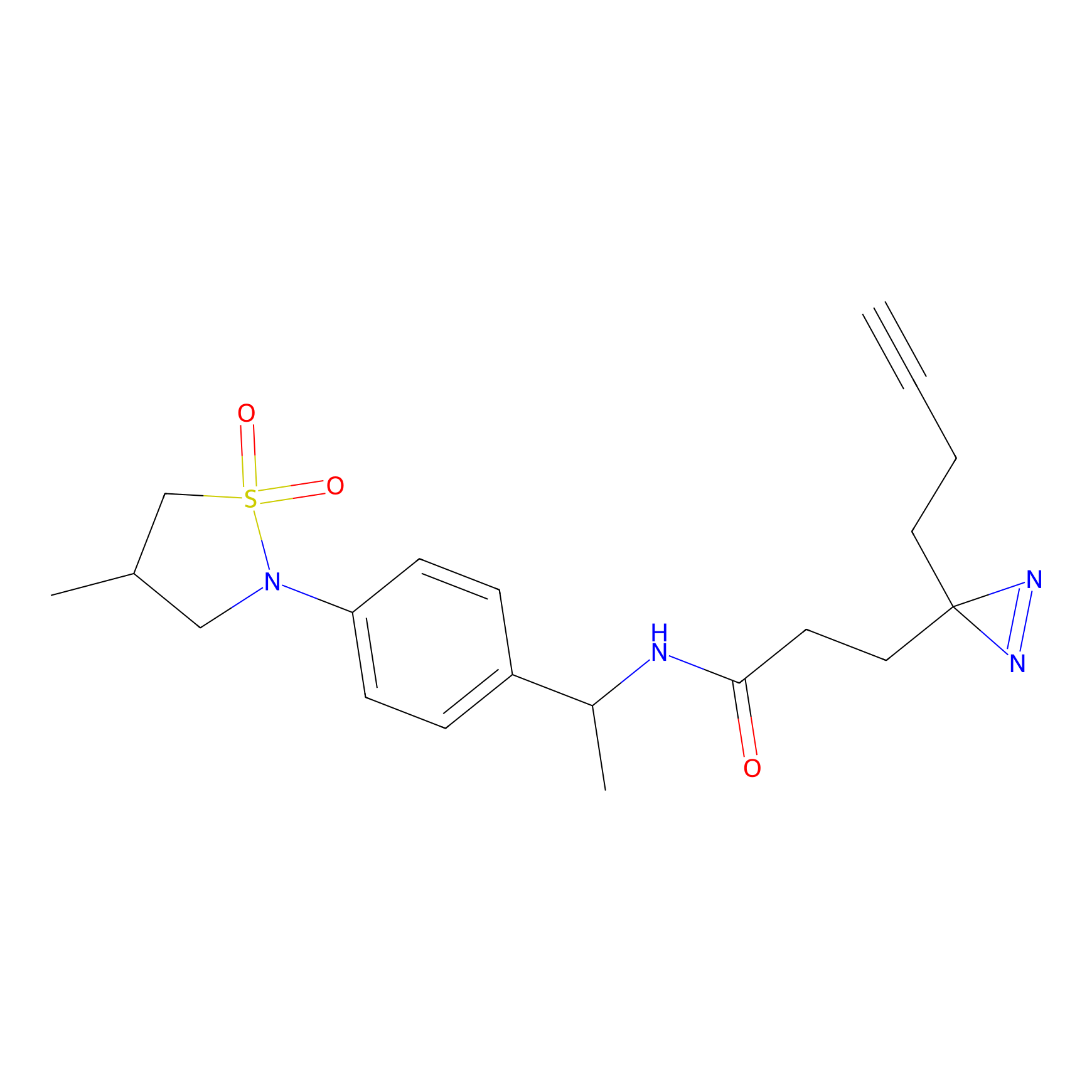
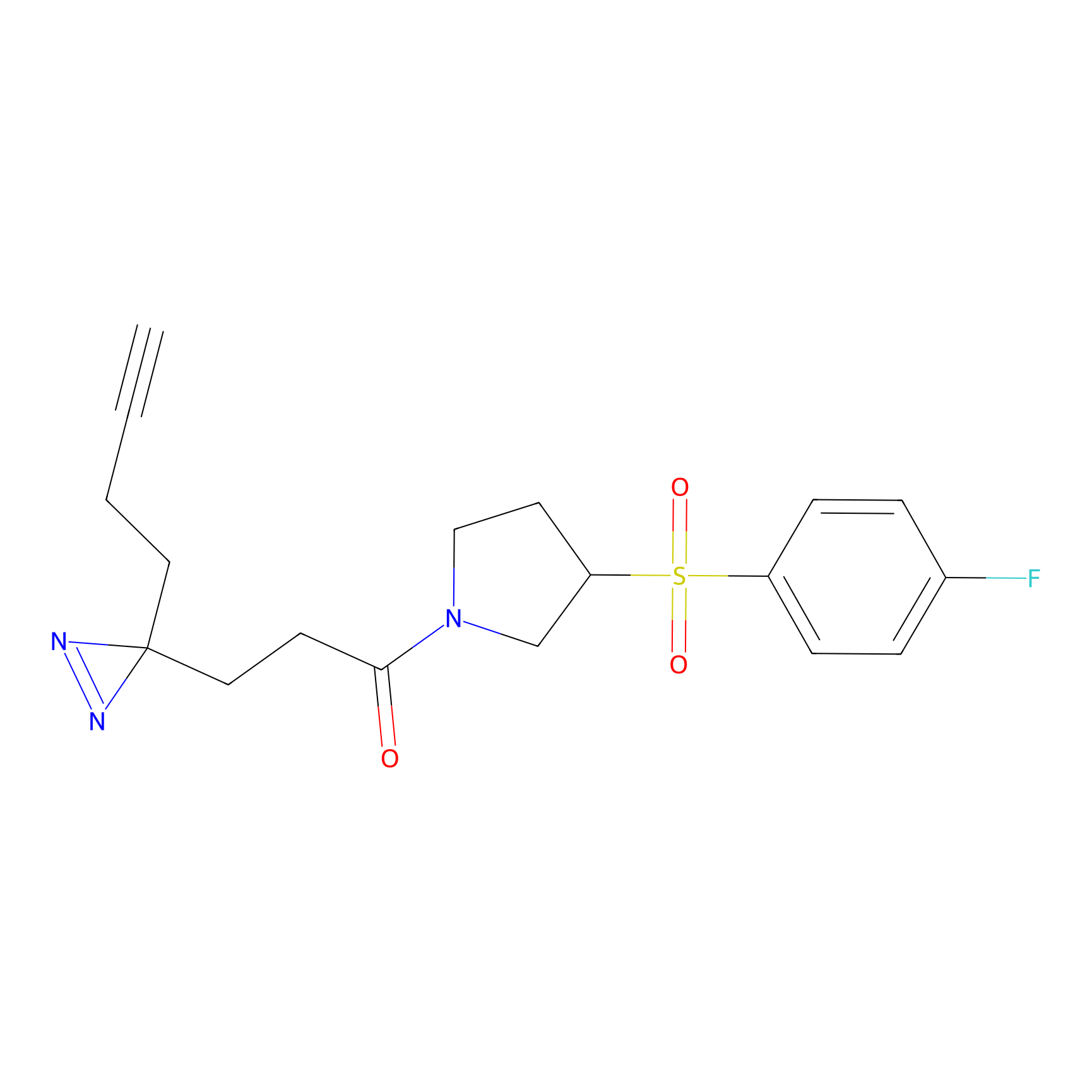
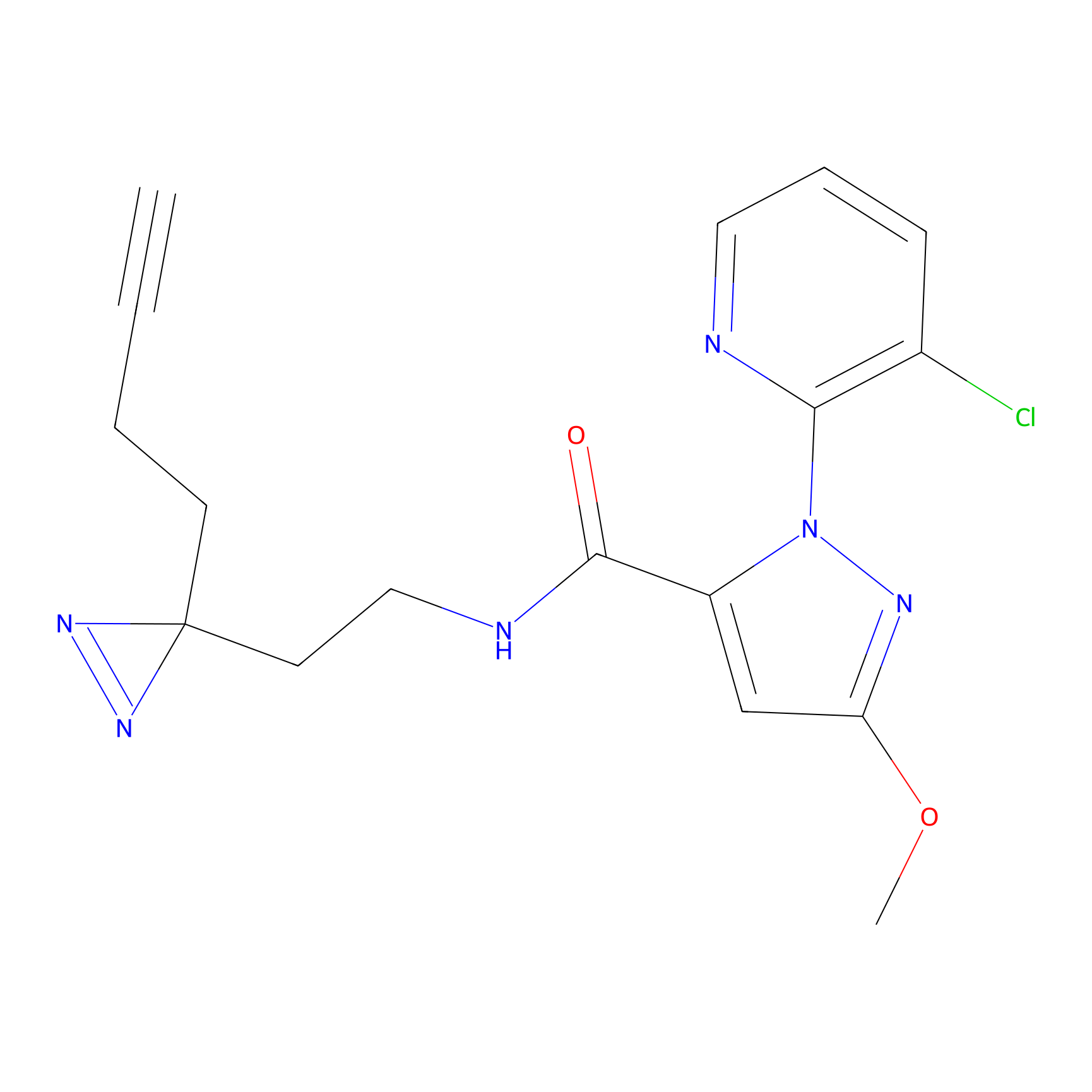
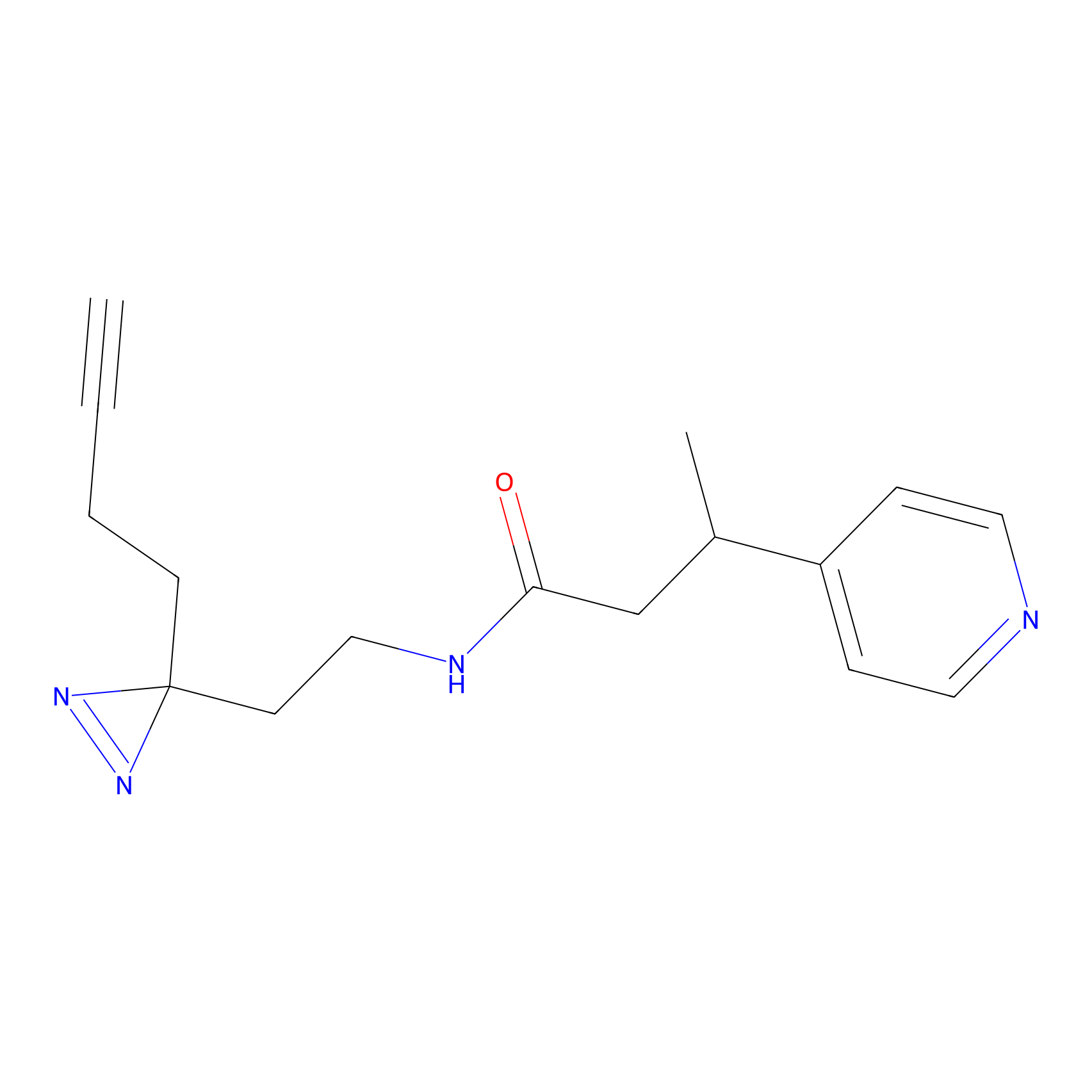
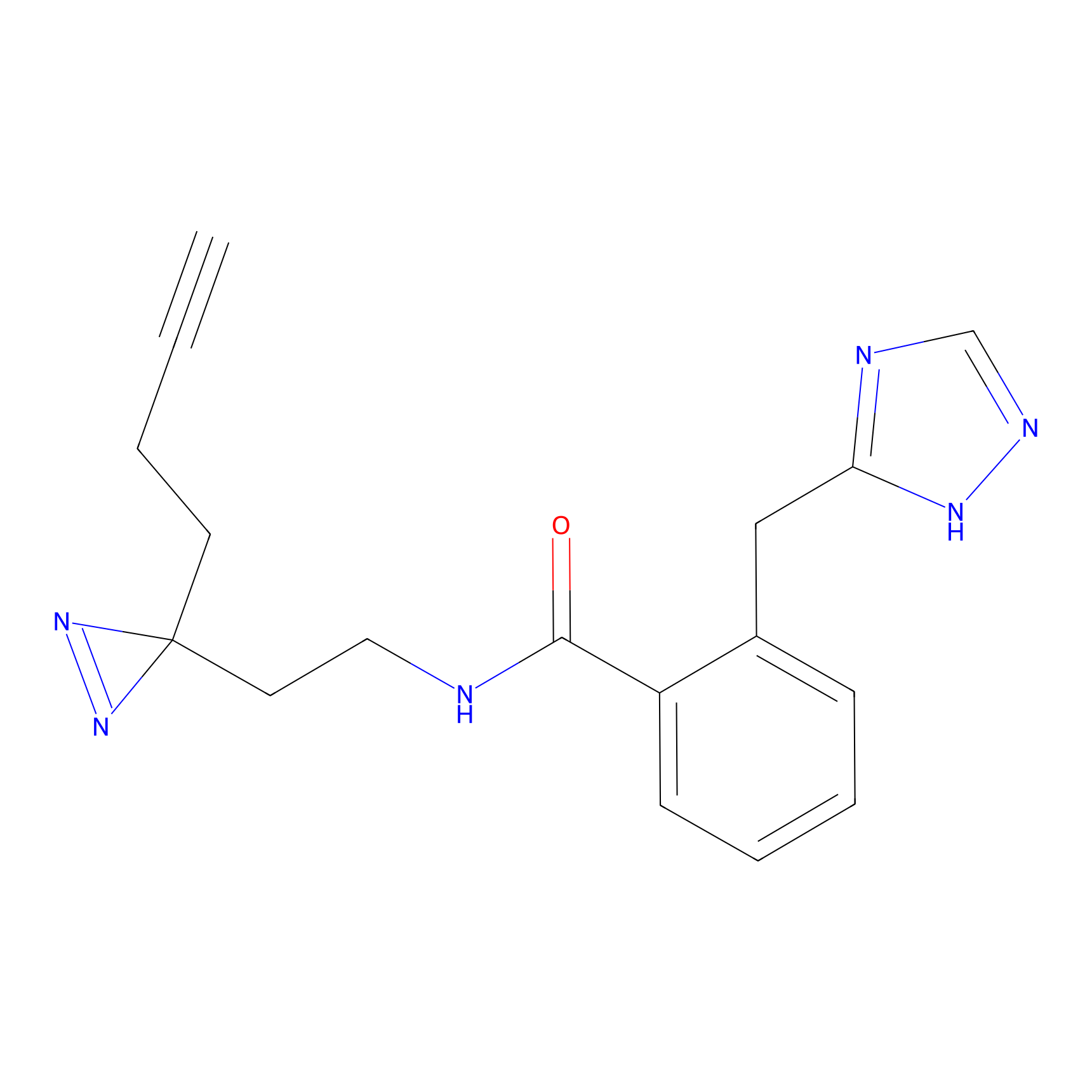
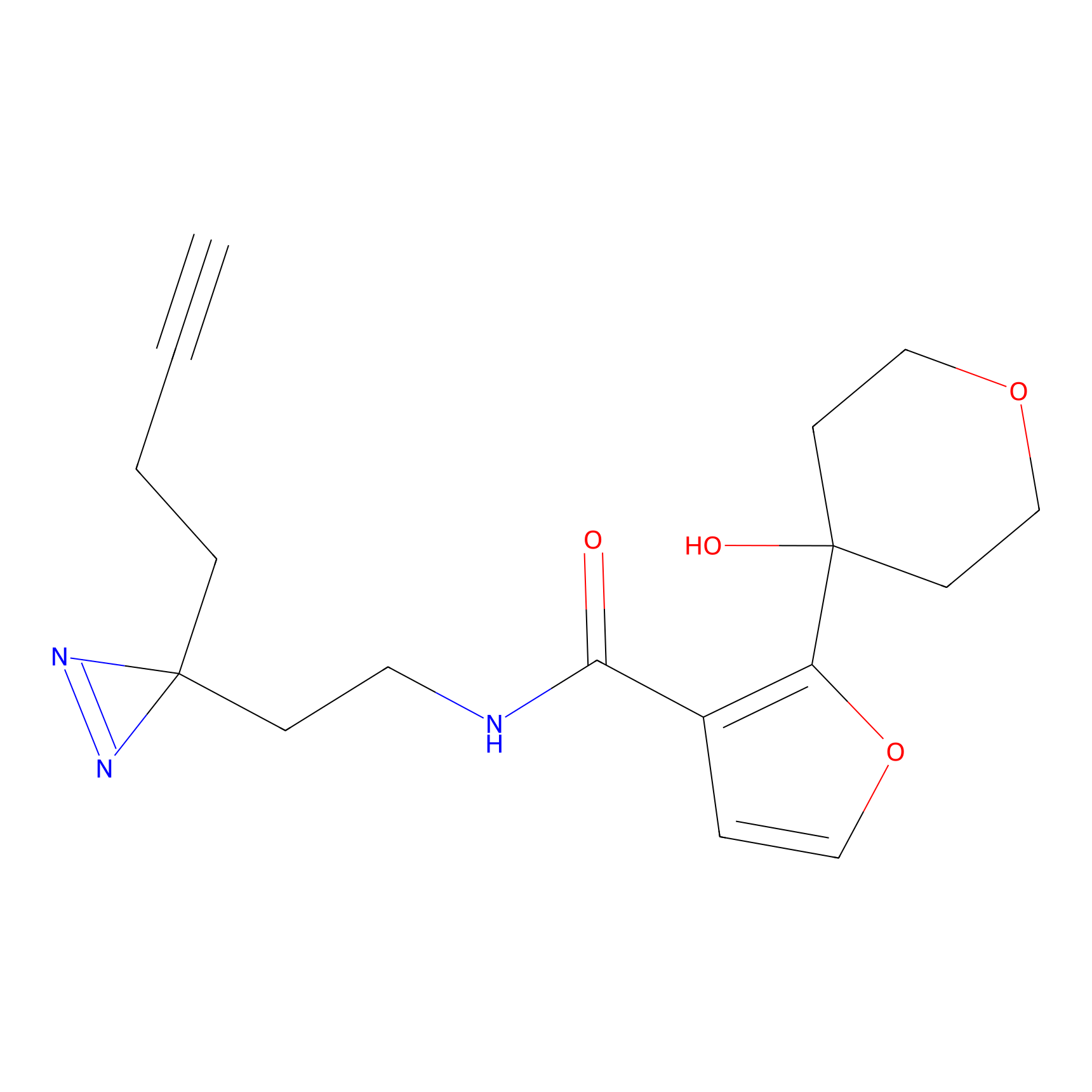
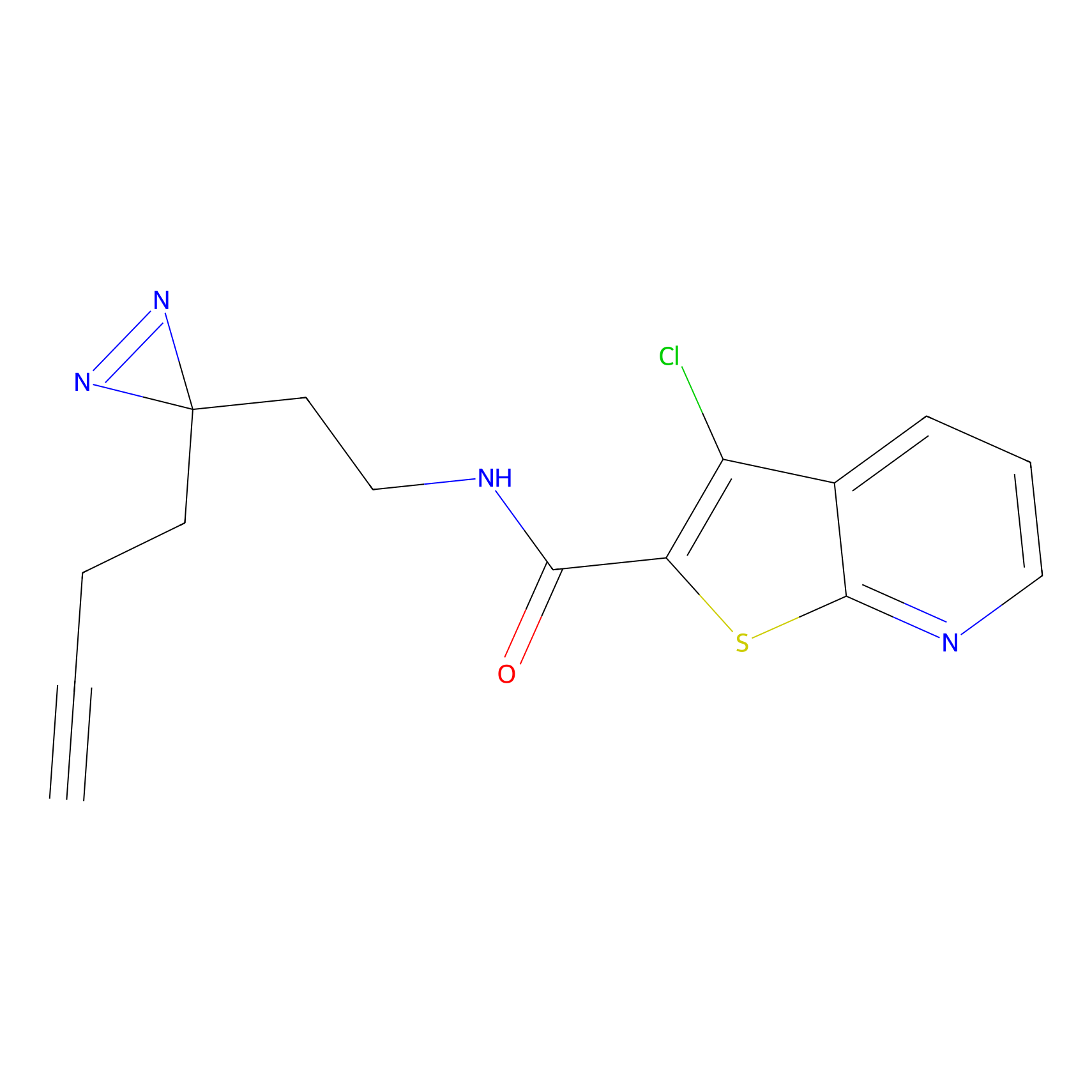
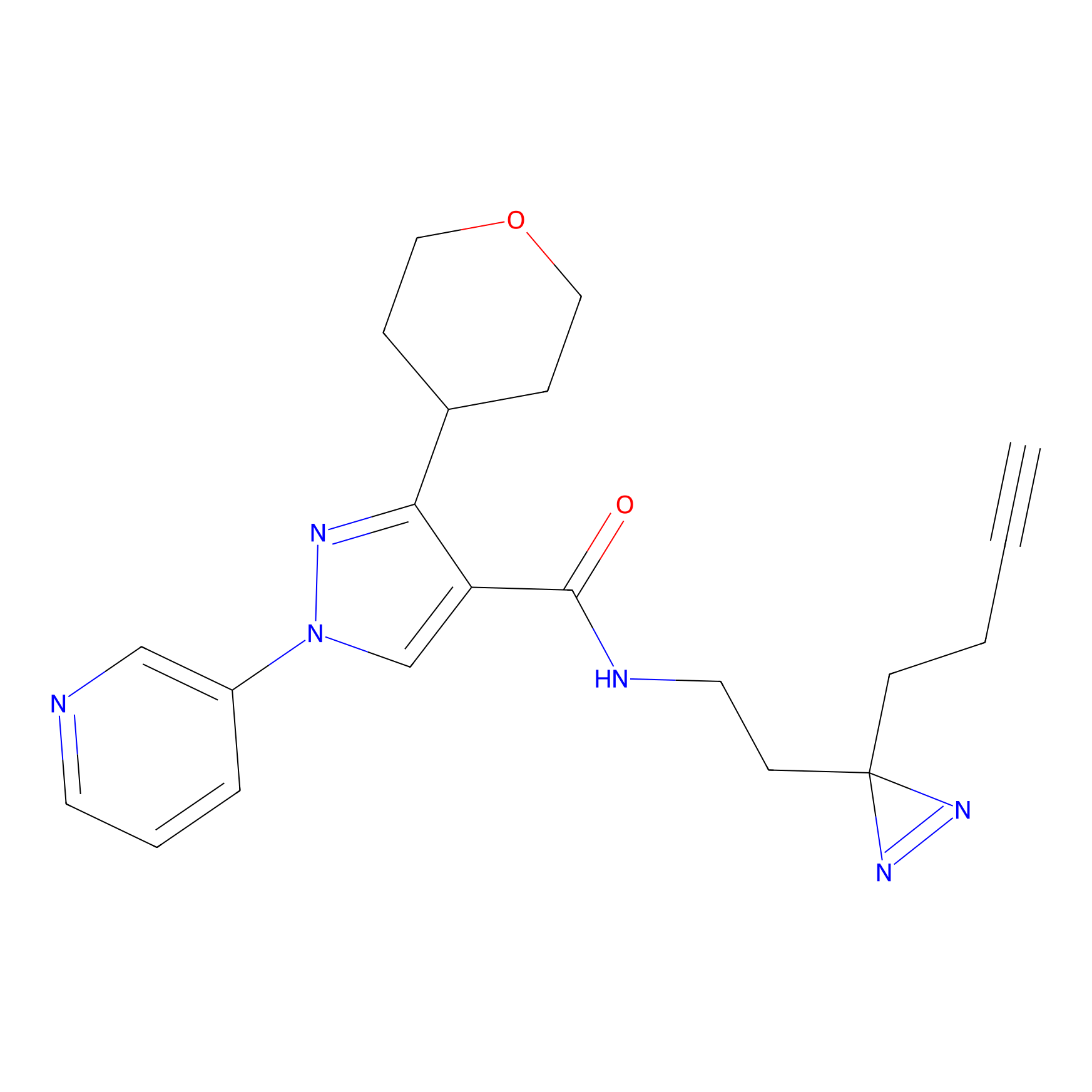
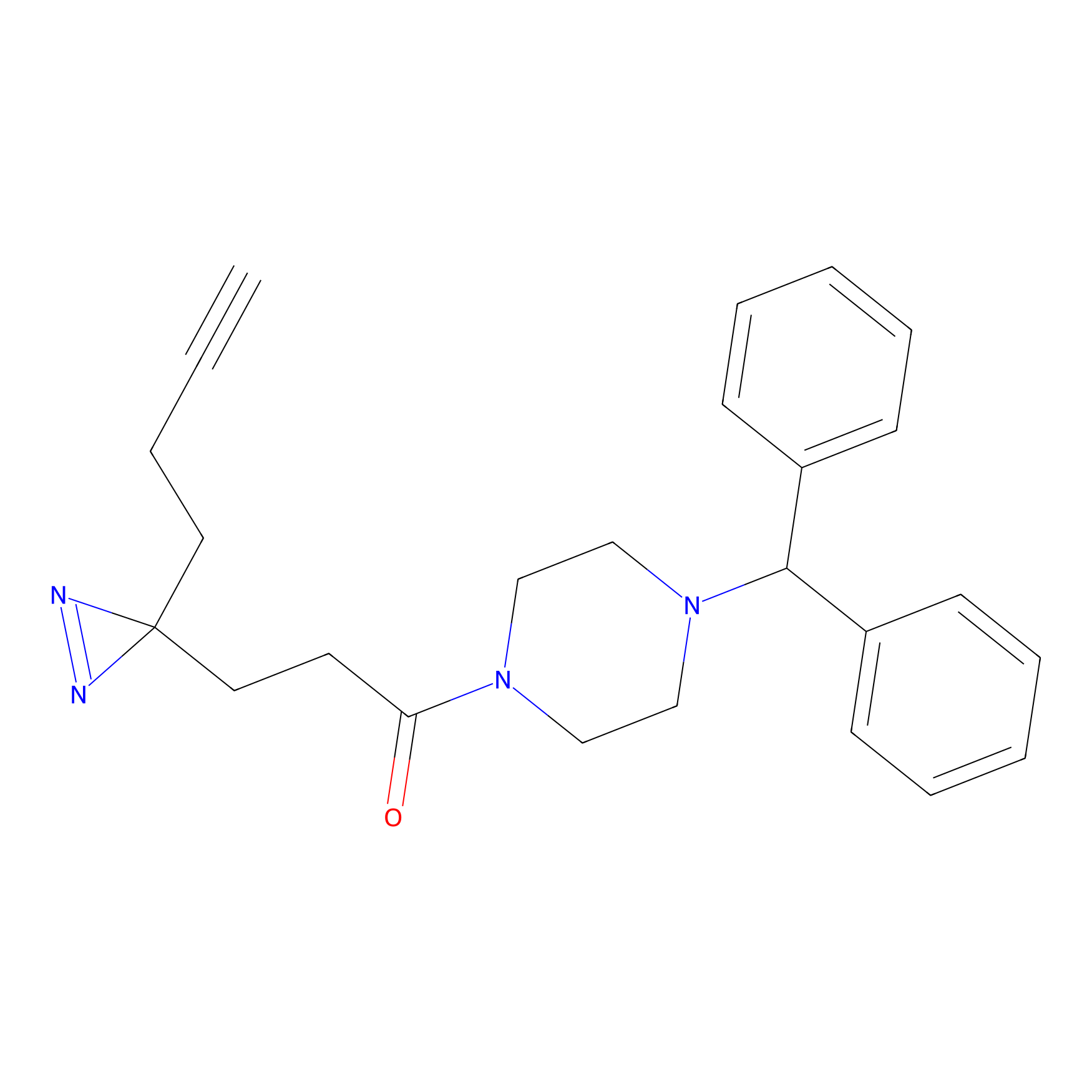
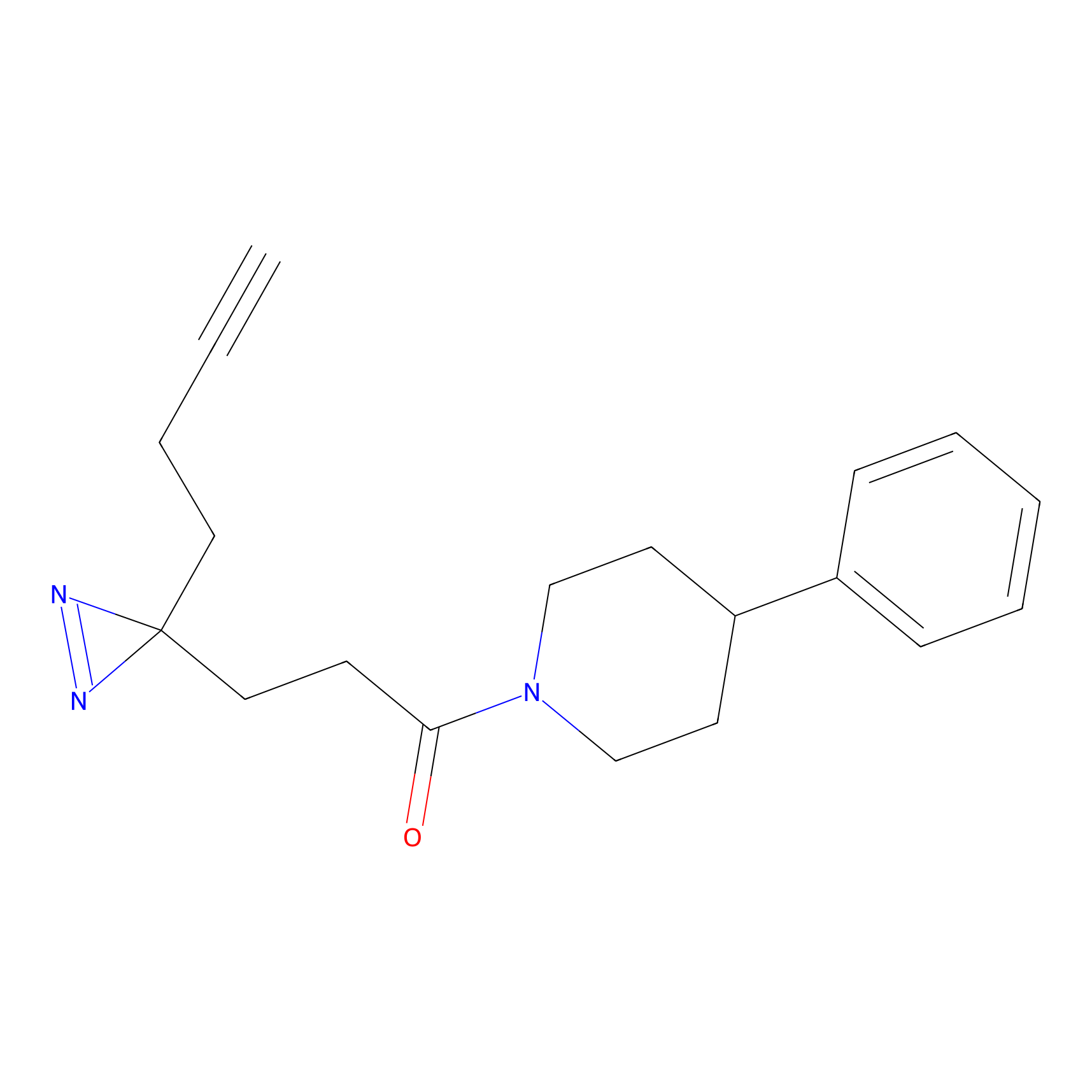
|
AOyne Probe Info |
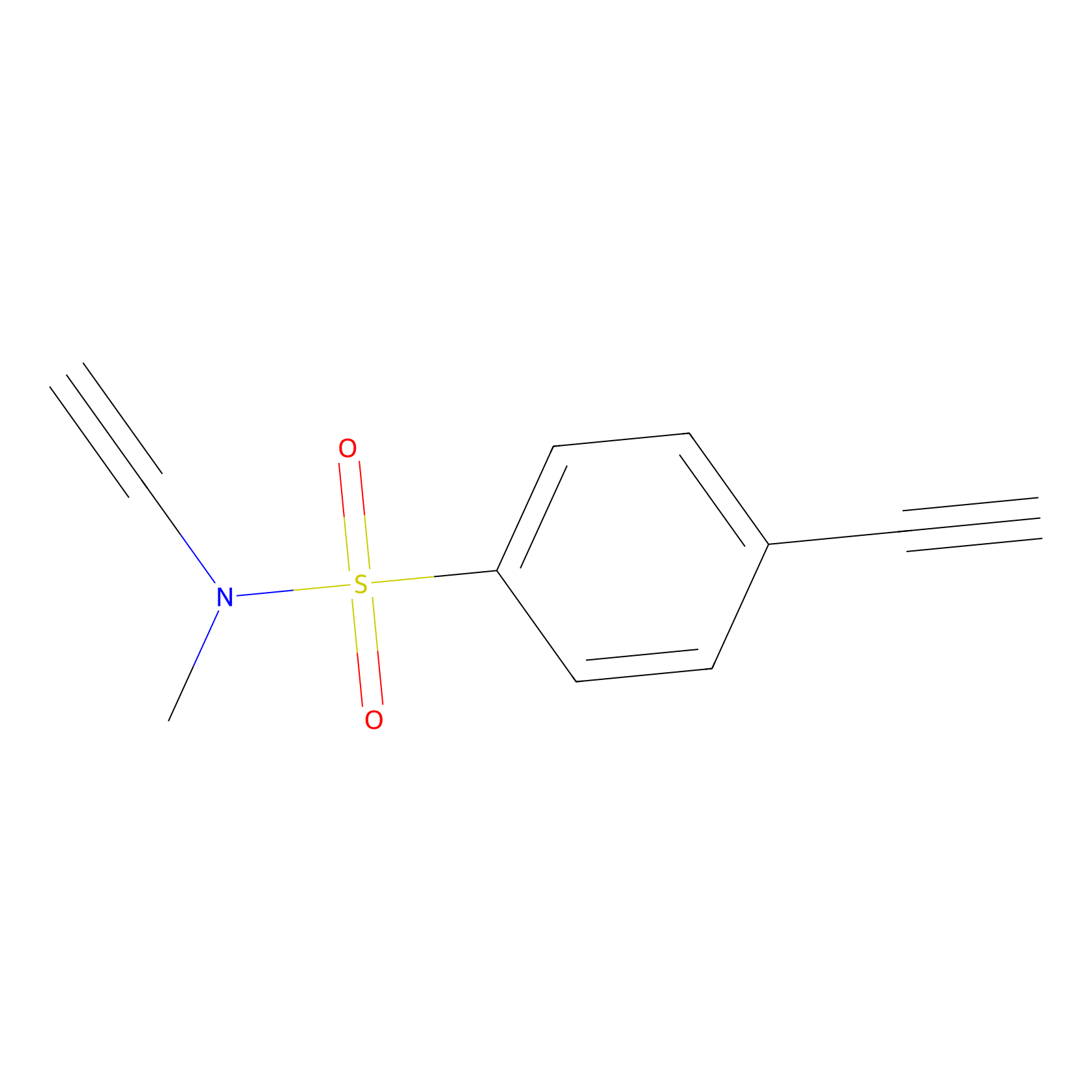
 |
15.00 | LDD0443 | [3] | |
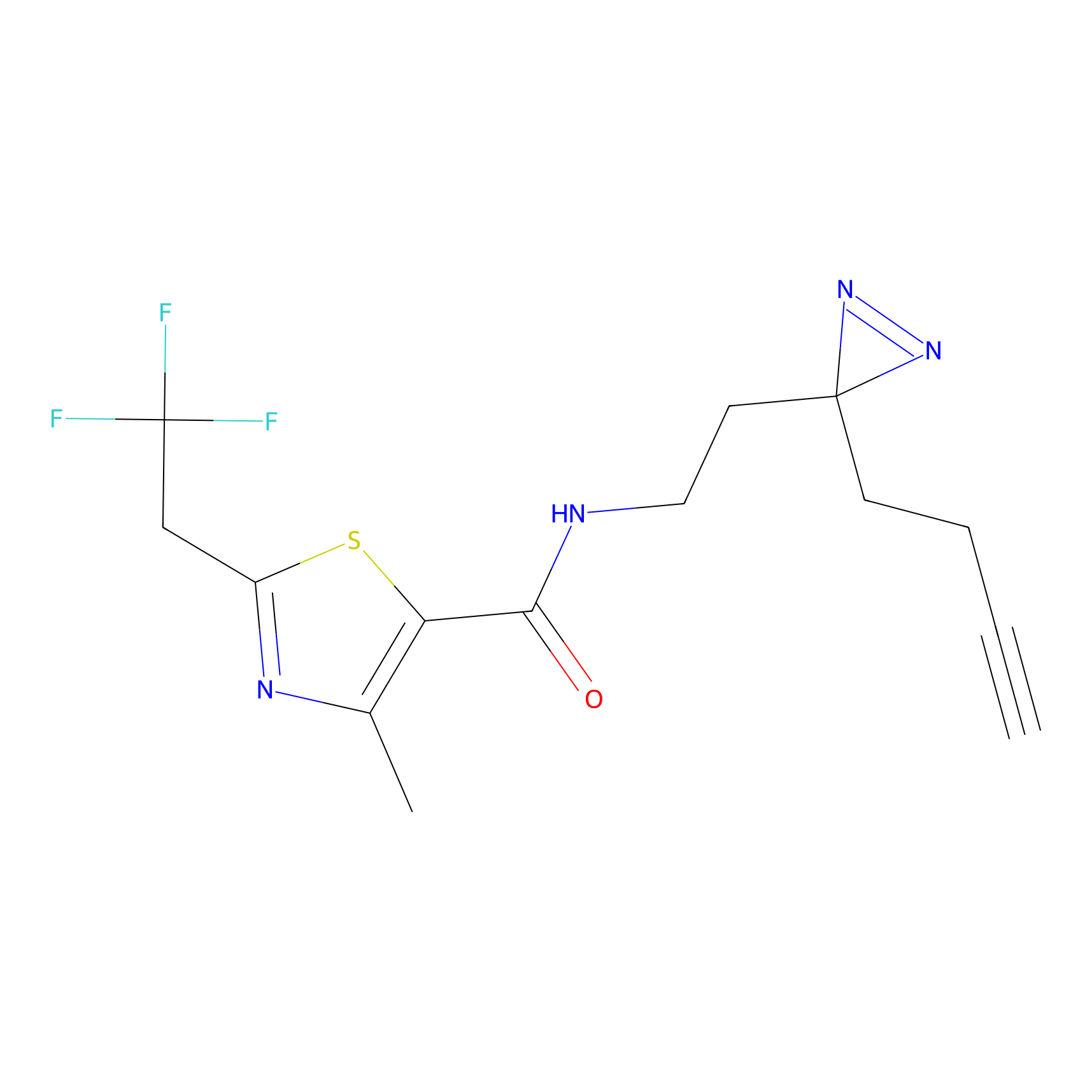
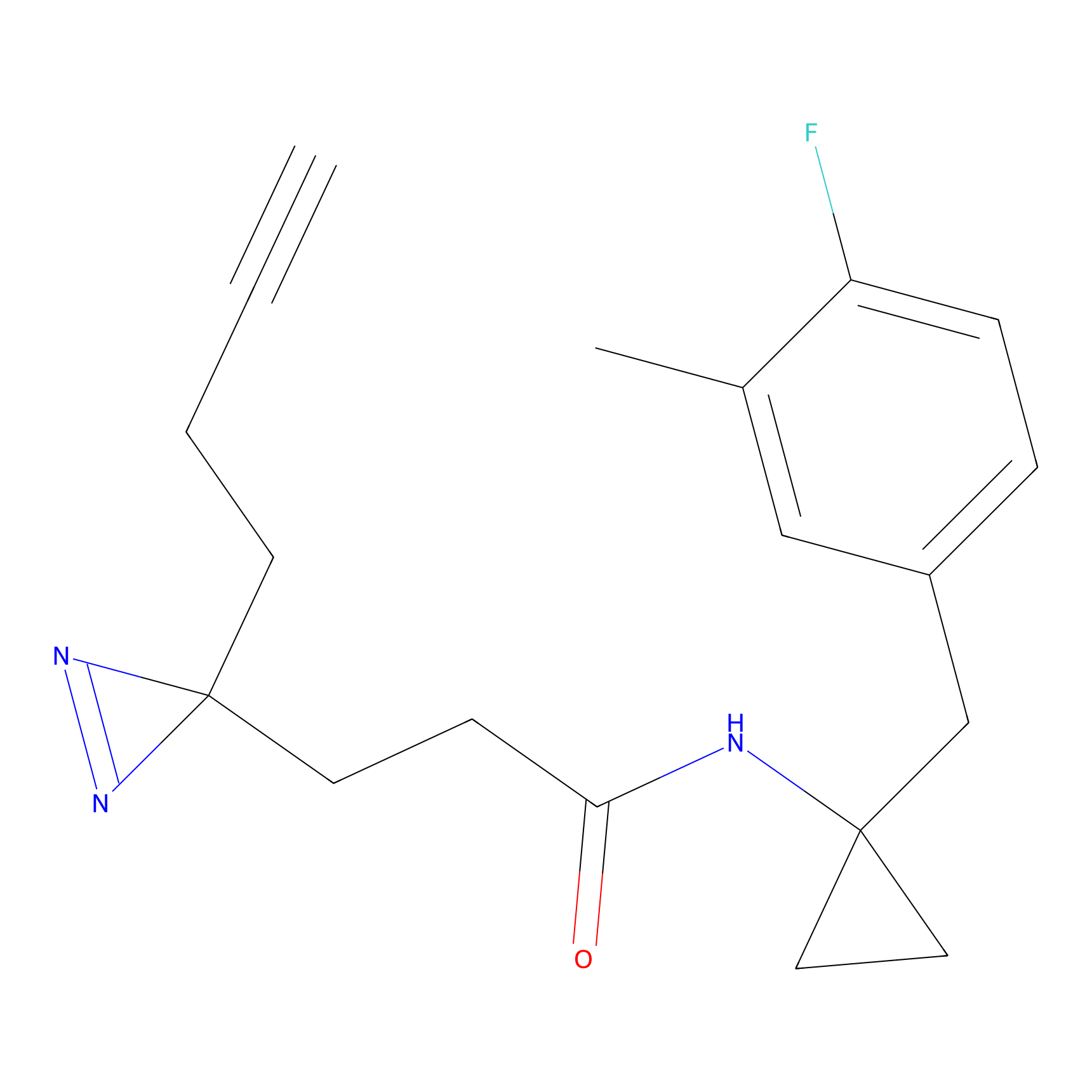
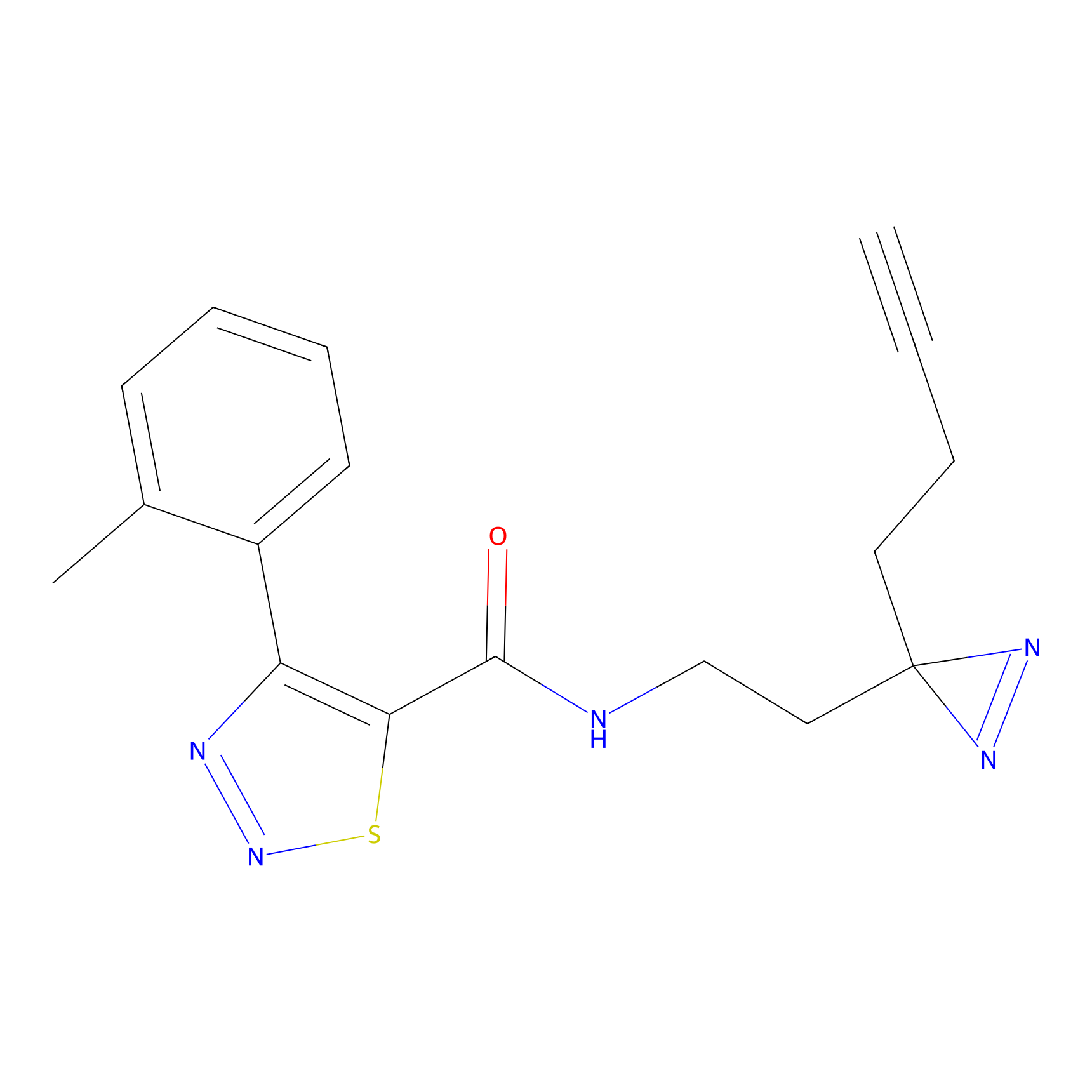
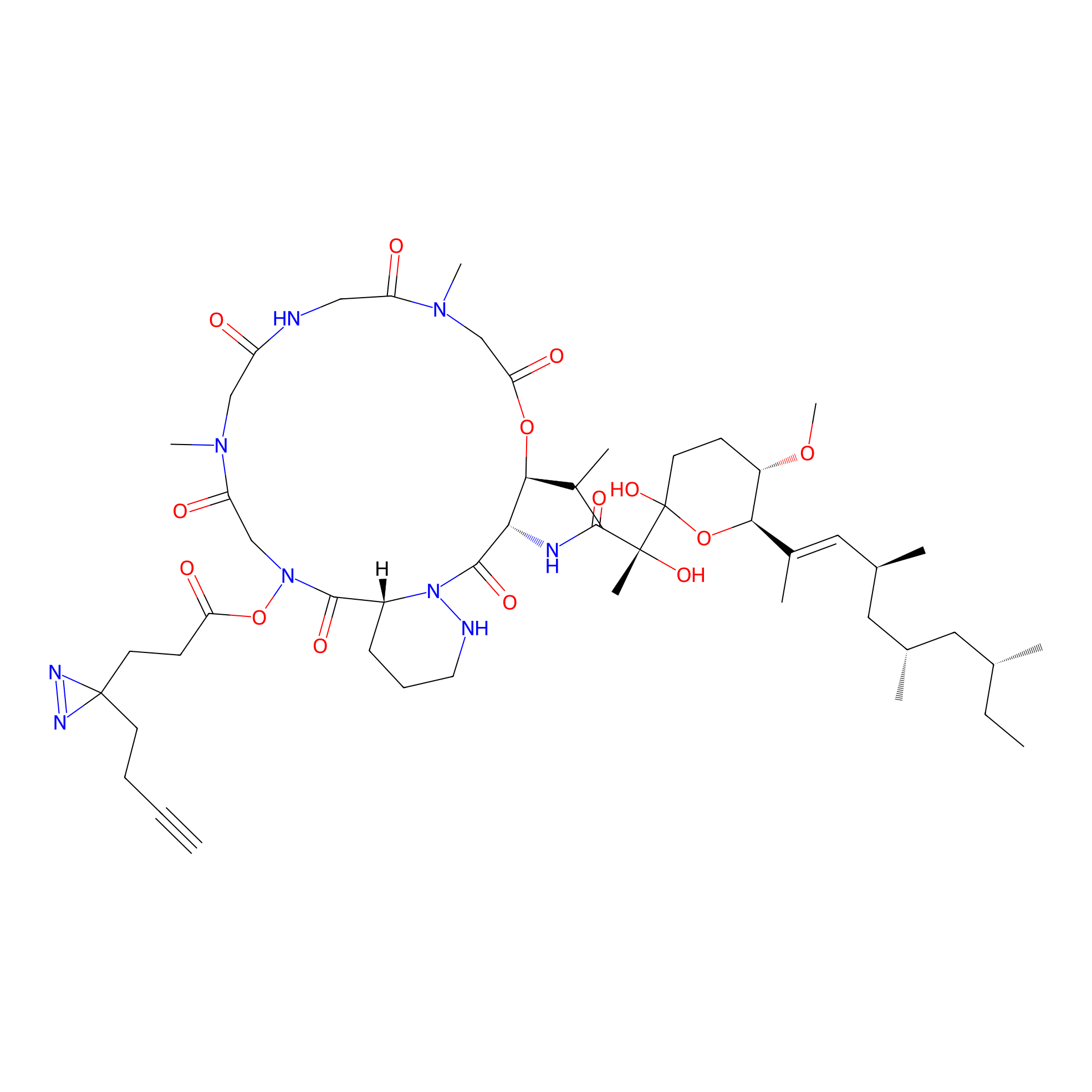
PAL-AfBPP Probe
References