Details of the Target
General Information of Target
| Target ID | LDTP13620 | |||||
|---|---|---|---|---|---|---|
| Target Name | Lysosomal thioesterase PPT2 (PPT2) | |||||
| Gene Name | PPT2 | |||||
| Gene ID | 9374 | |||||
| Synonyms |
Lysosomal thioesterase PPT2; PPT-2; EC 3.1.2.-; S-thioesterase G14 |
|||||
| 3D Structure | ||||||
| Sequence |
MEFTASPKPQLSSRANAFSIAALMSSGGSKEKEATENTIKPLEQFVEKSSCAQPLGELTS
LDAHGEFGGGSGSSPSSSSLCTEPLIPTTPIIPSEEMAKIACSLETKELWDKFHELGTEM IITKSGRRMFPTIRVSFSGVDPEAKYIVLMDIVPVDNKRYRYAYHRSSWLVAGKADPPLP ARLYVHPDSPFTGEQLLKQMVSFEKVKLTNNELDQHGHIILNSMHKYQPRVHIIKKKDHT ASLLNLKSEEFRTFIFPETVFTAVTAYQNQLITKLKIDSNPFAKGFRDSSRLTDIERESV ESLIQKHSYARSPIRTYGGEEDVLGDESQTTPNRGSAFTTSDNLSLSSWVSSSSSFPGFQ HPQSLTALGTSTASIATPIPHPIQGSLPPYSRLGMPLTPSAIASSMQGSGPTFPSFHMPR YHHYFQQGPYAAIQGLRHSSAVMTPFV |
|||||
| Target Bioclass |
Enzyme
|
|||||
| Family |
Palmitoyl-protein thioesterase family
|
|||||
| Subcellular location |
Lysosome
|
|||||
| Function |
Removes thioester-linked fatty acyl groups from various substrates including S-palmitoyl-CoA. Has the highest S-thioesterase activity for the acyl groups palmitic and myristic acid followed by other short- and long-chain acyl substrates. However, because of structural constraints, is unable to remove palmitate from peptides or proteins.
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
| ChEMBL ID | ||||||
Target Site Mutations in Different Cell Lines
Probe(s) Labeling This Target
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
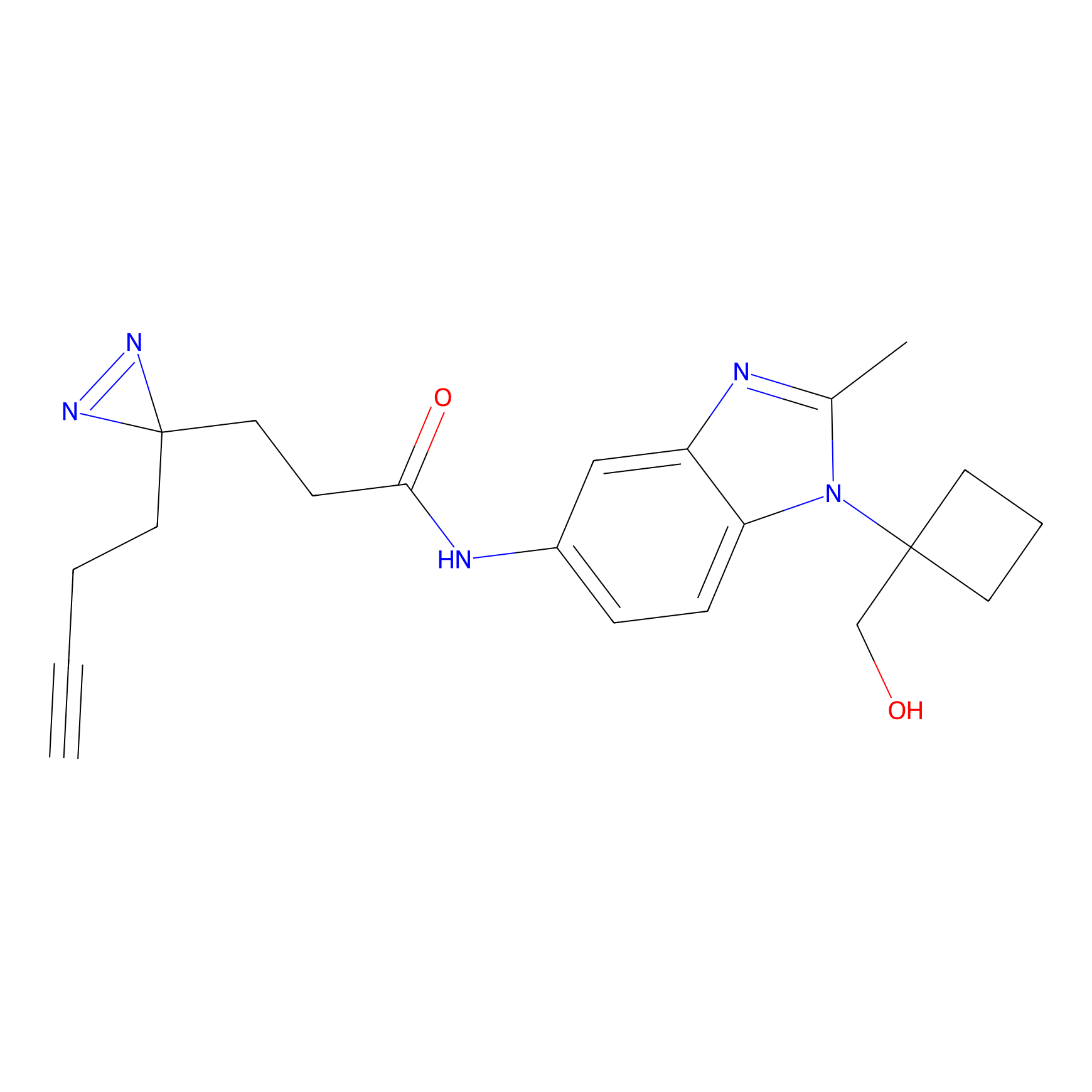
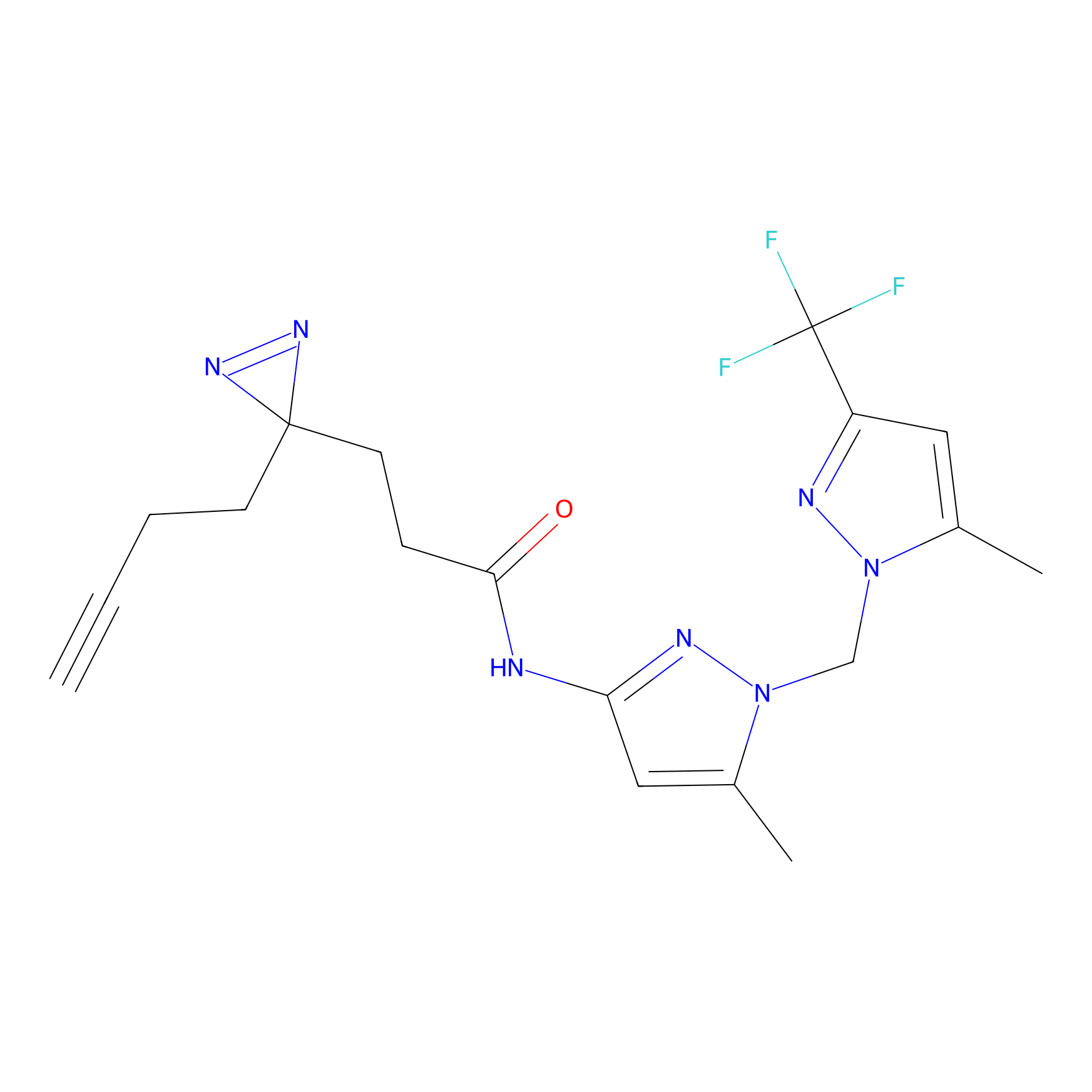
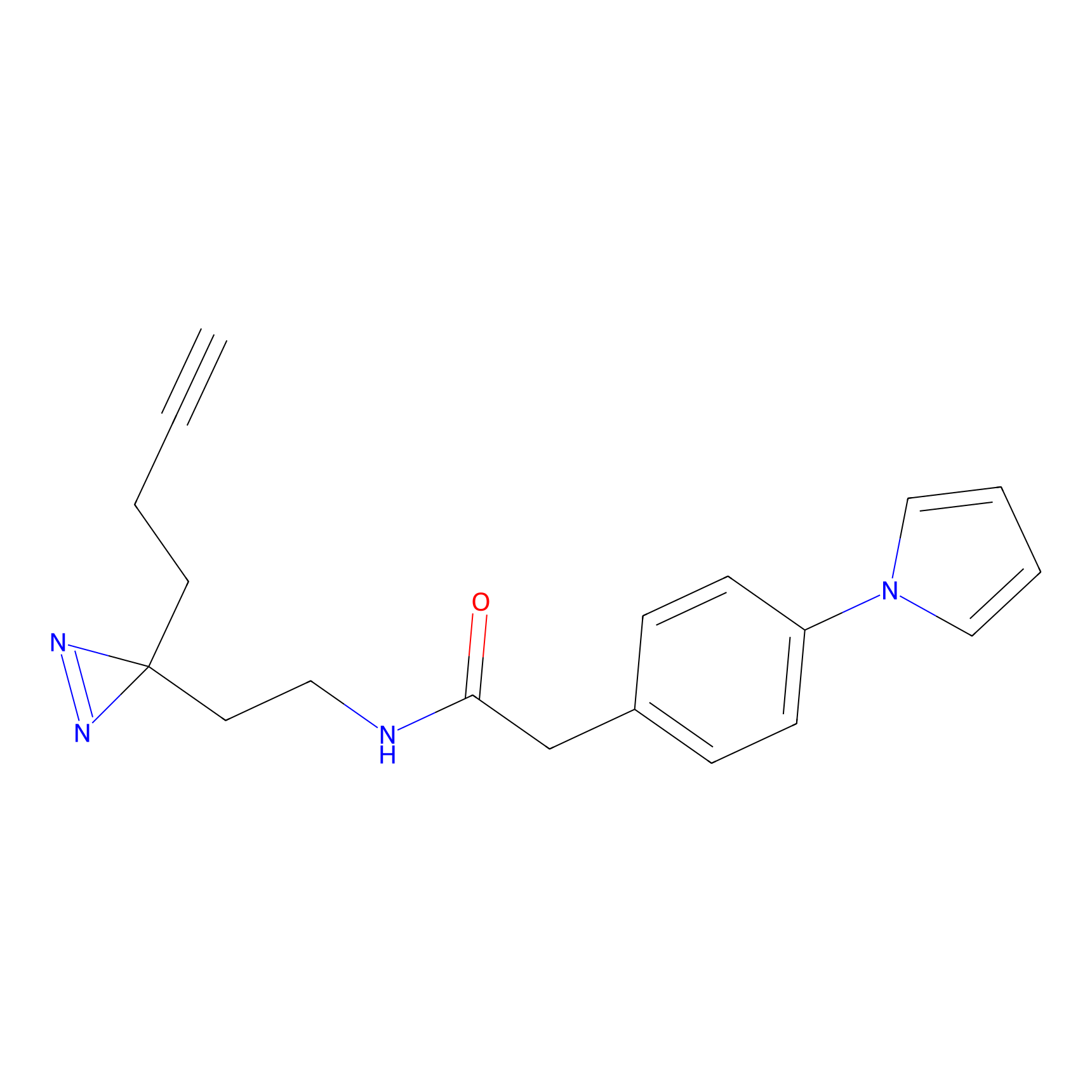
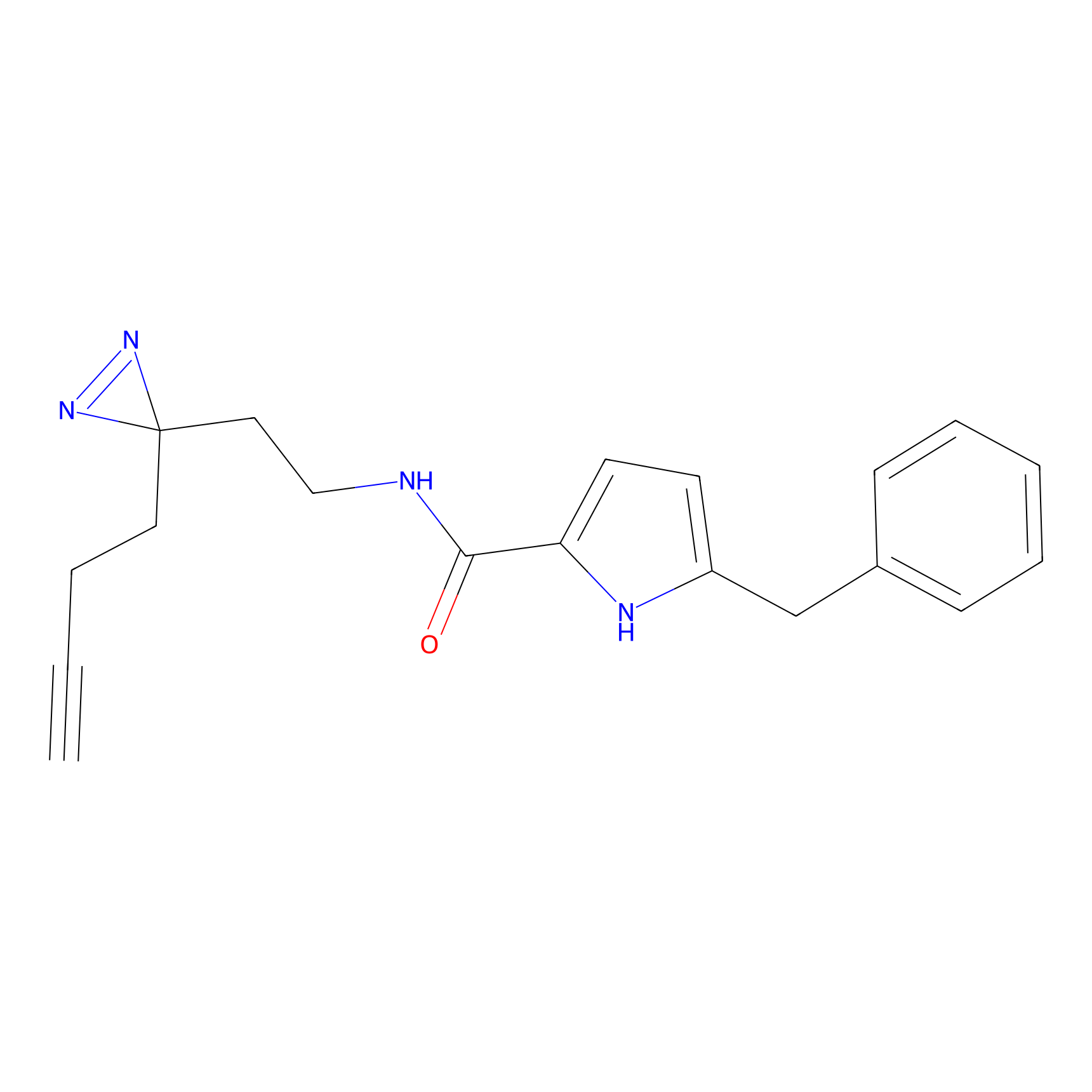
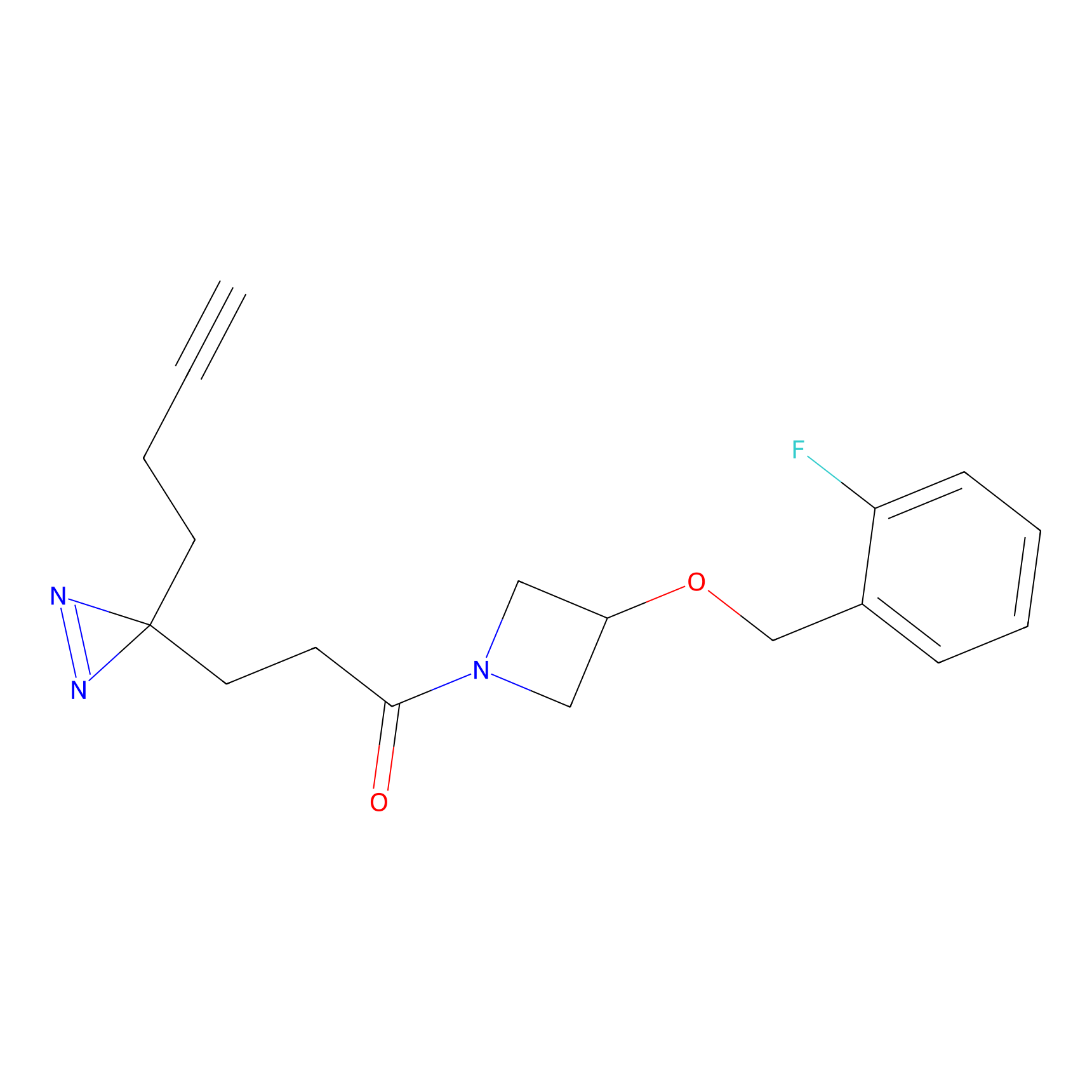
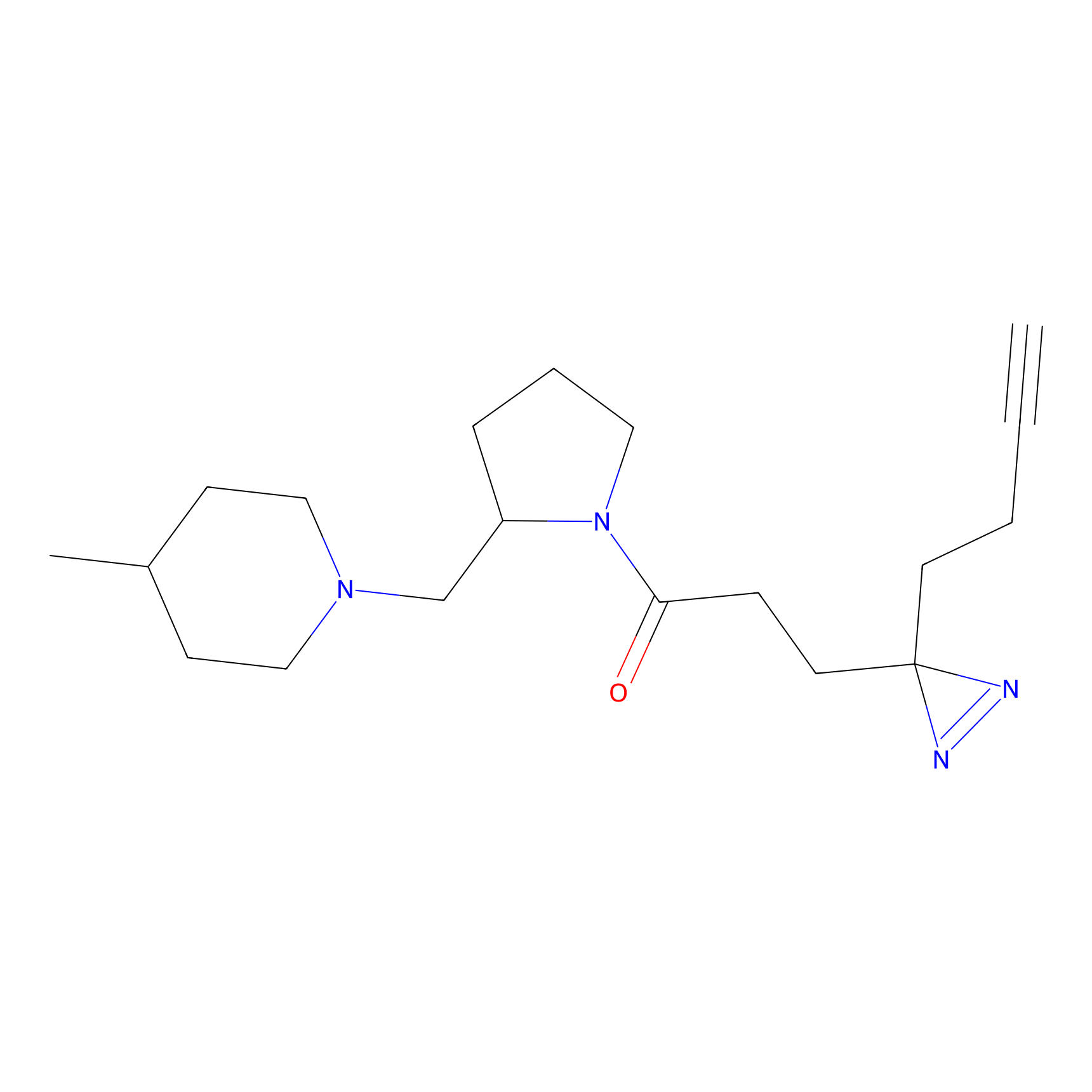
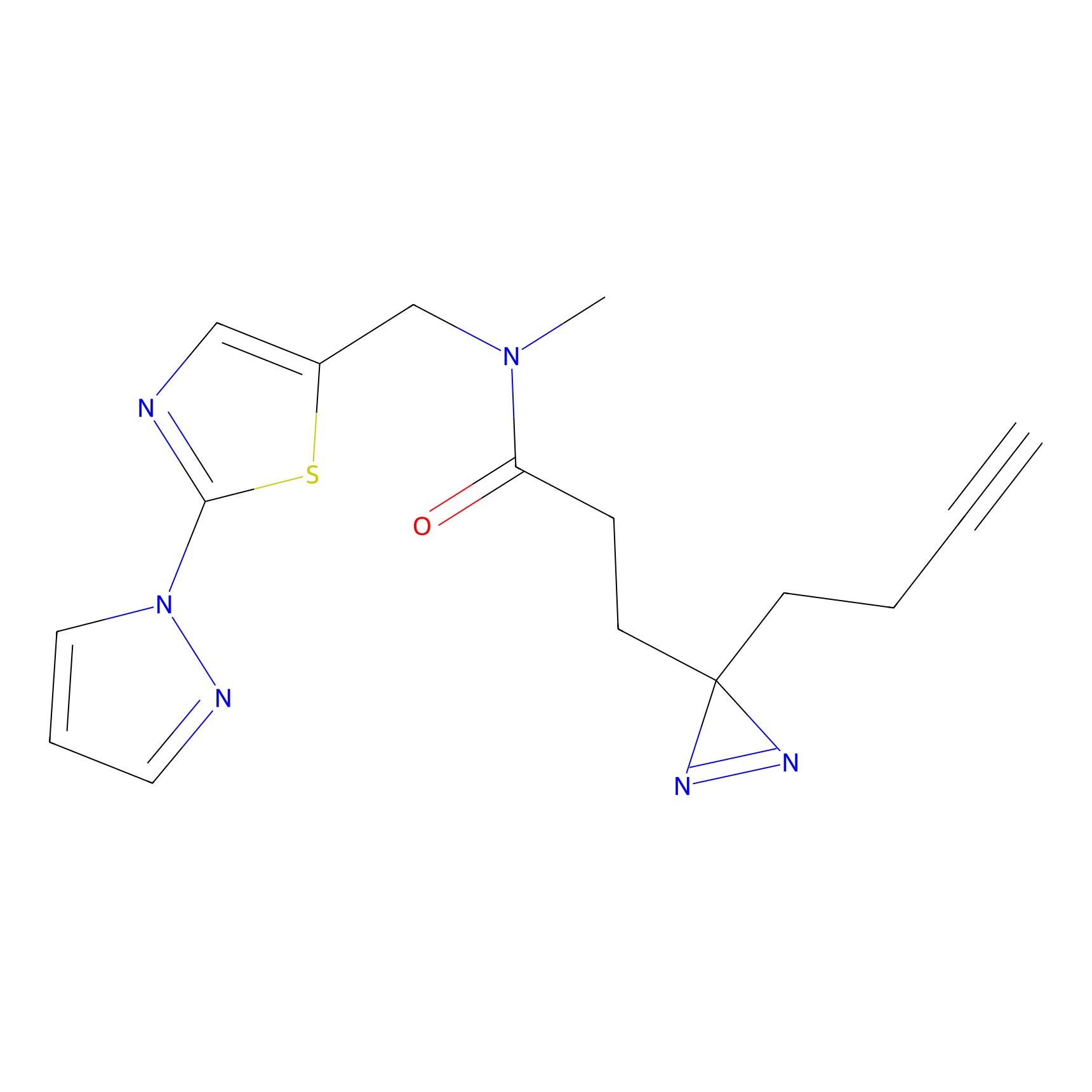
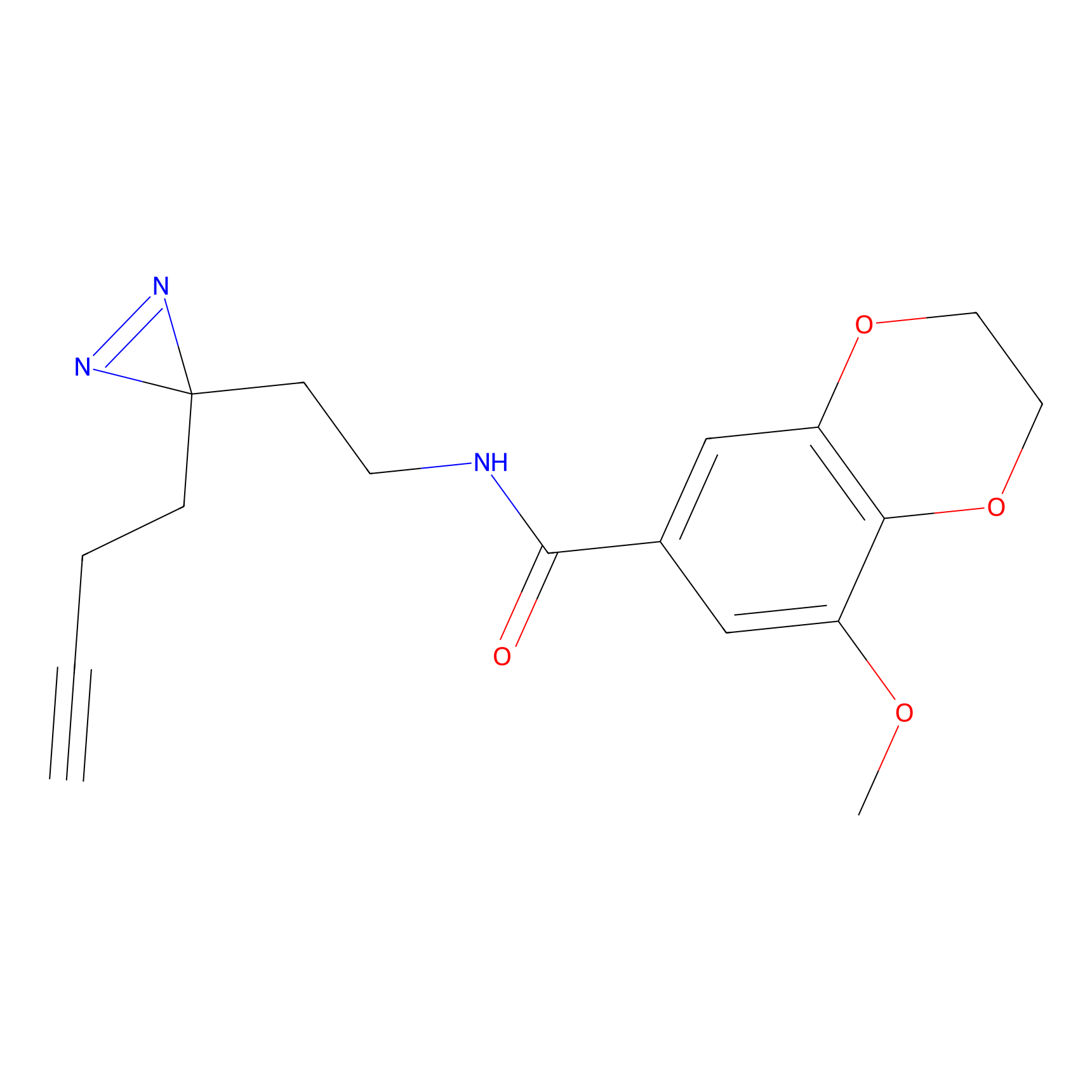
|
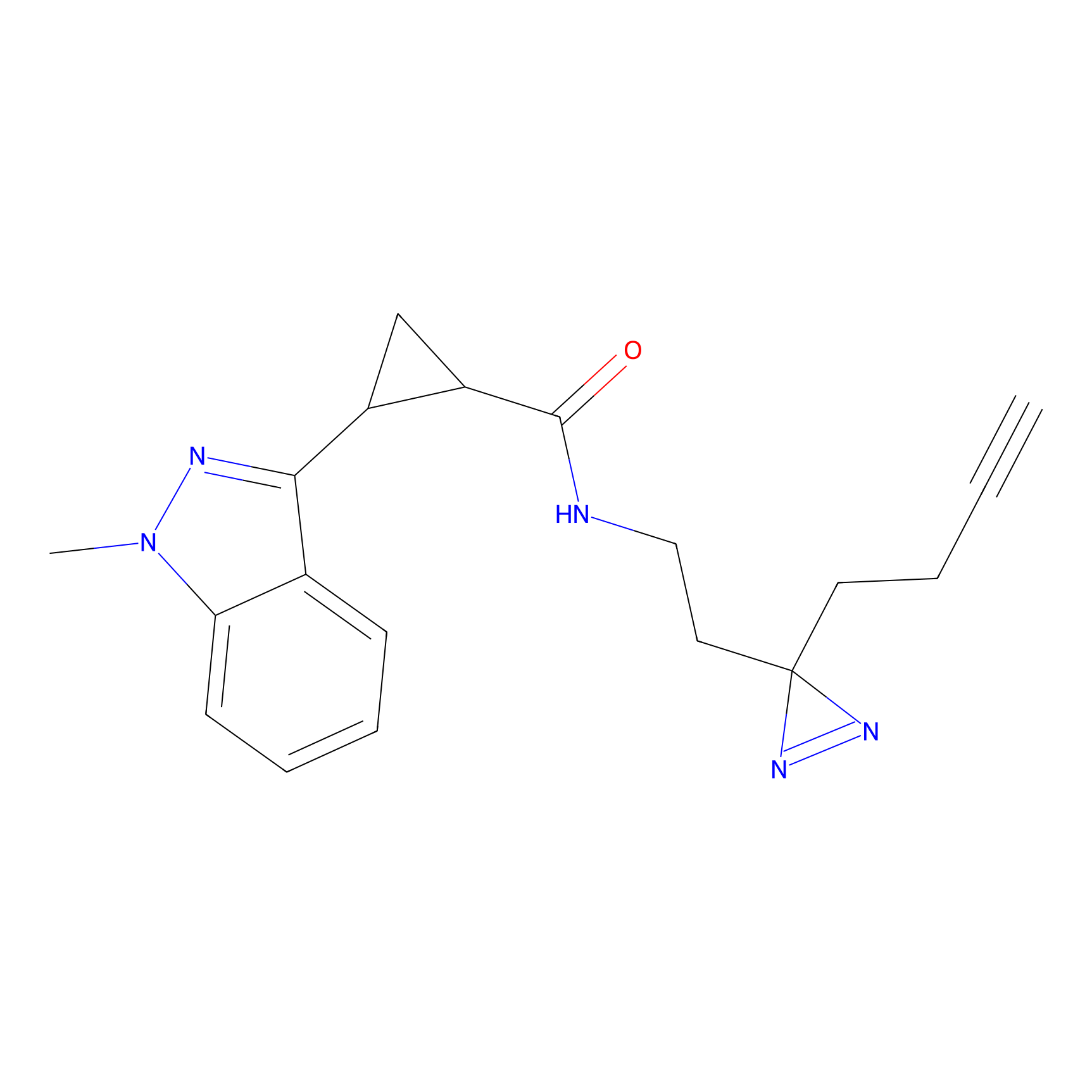
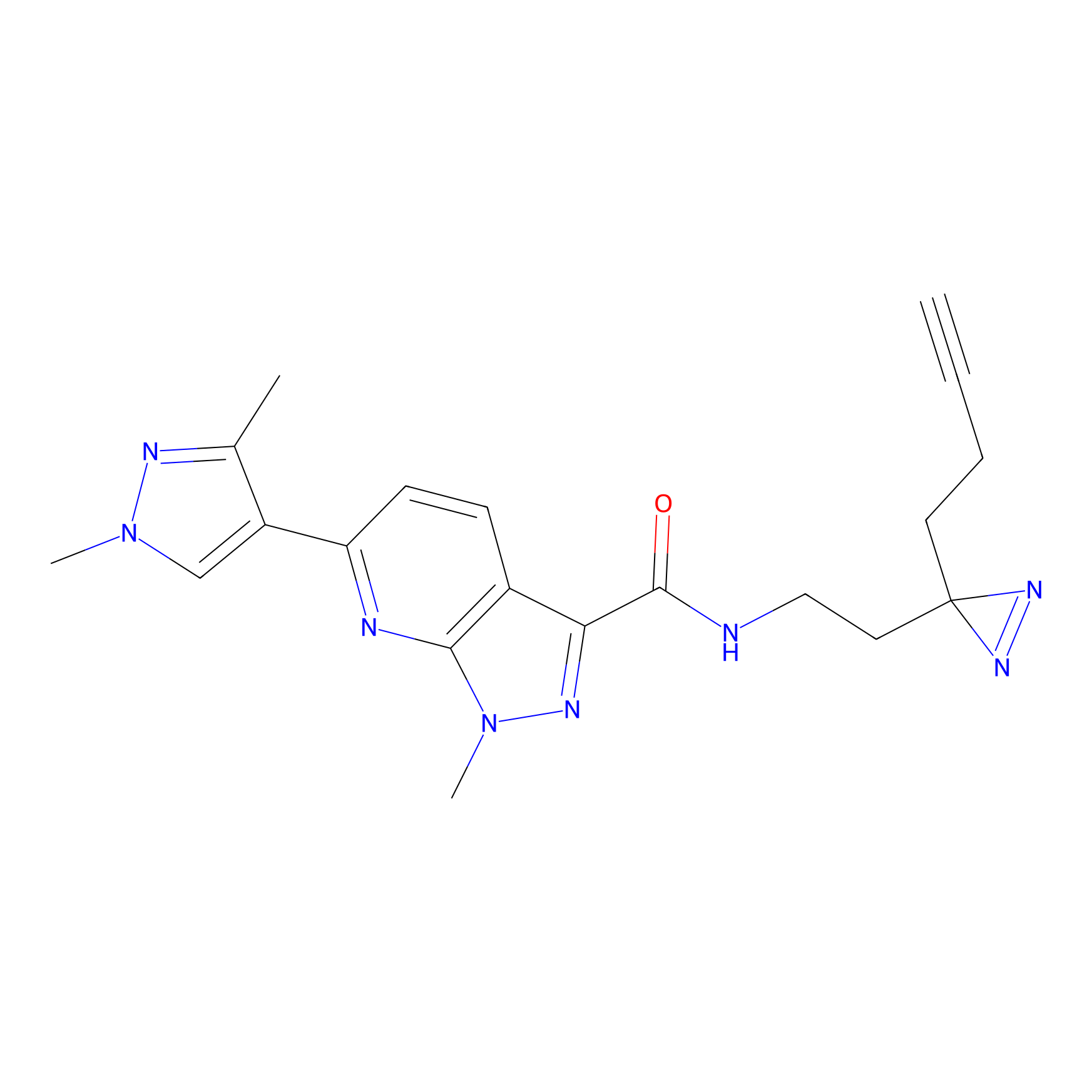
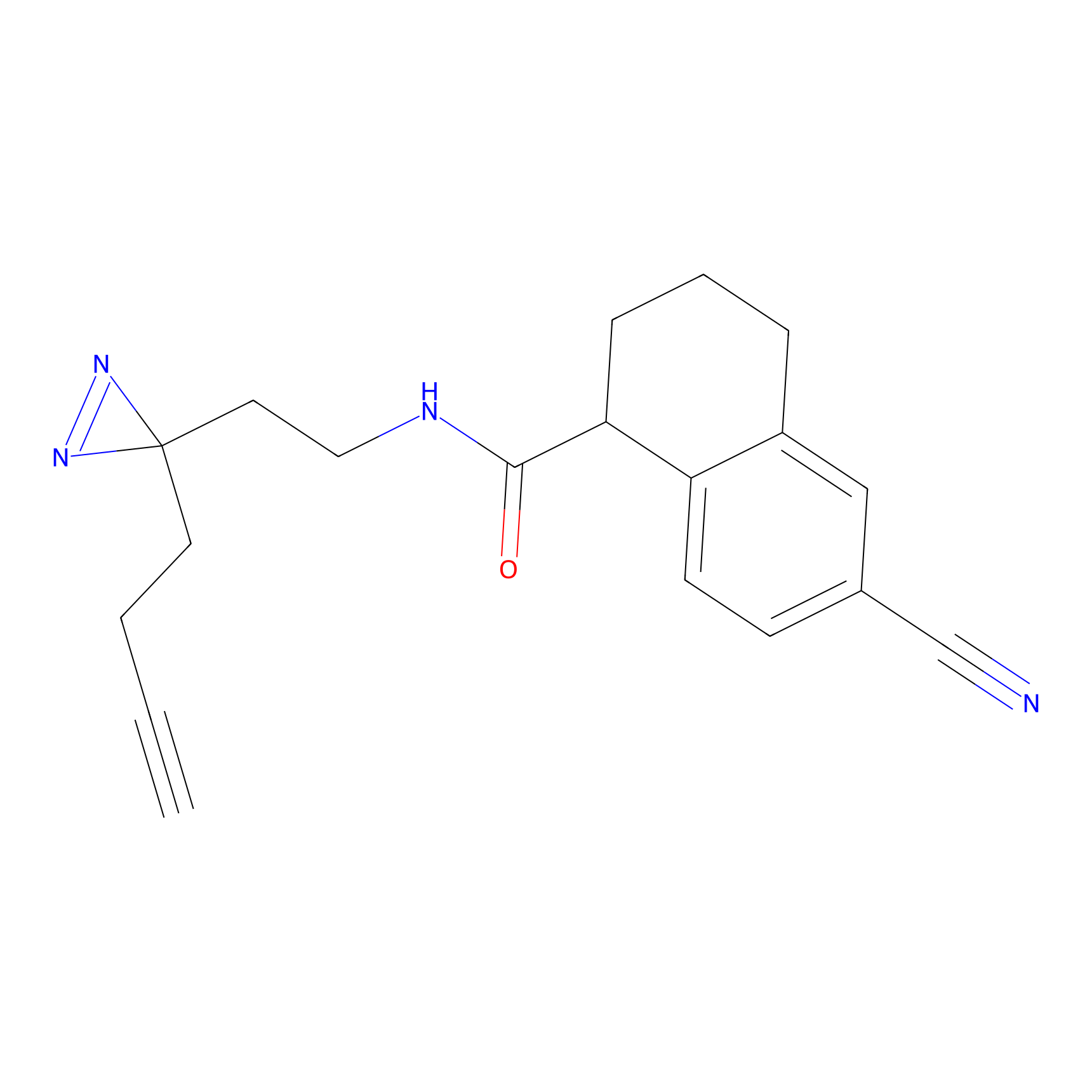
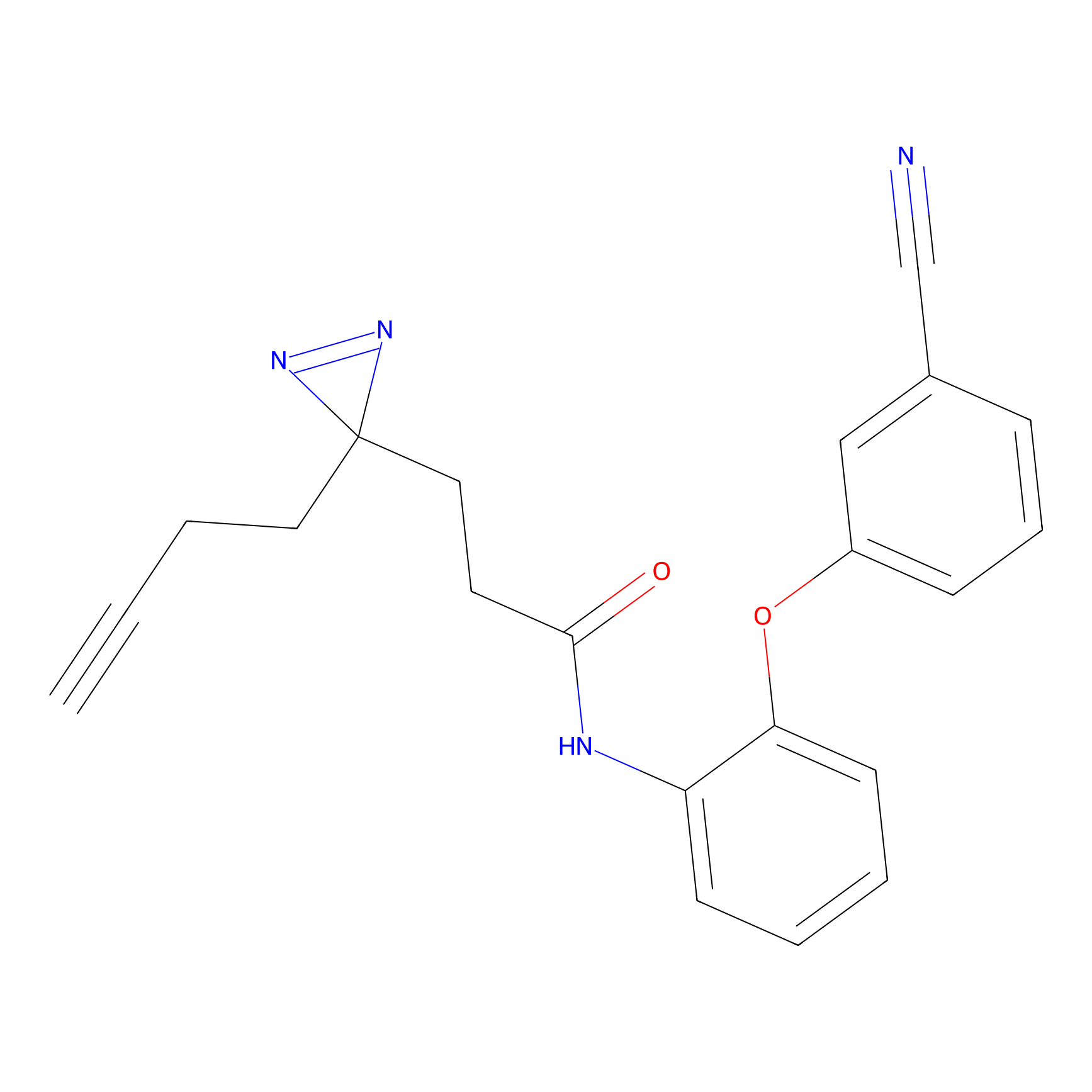
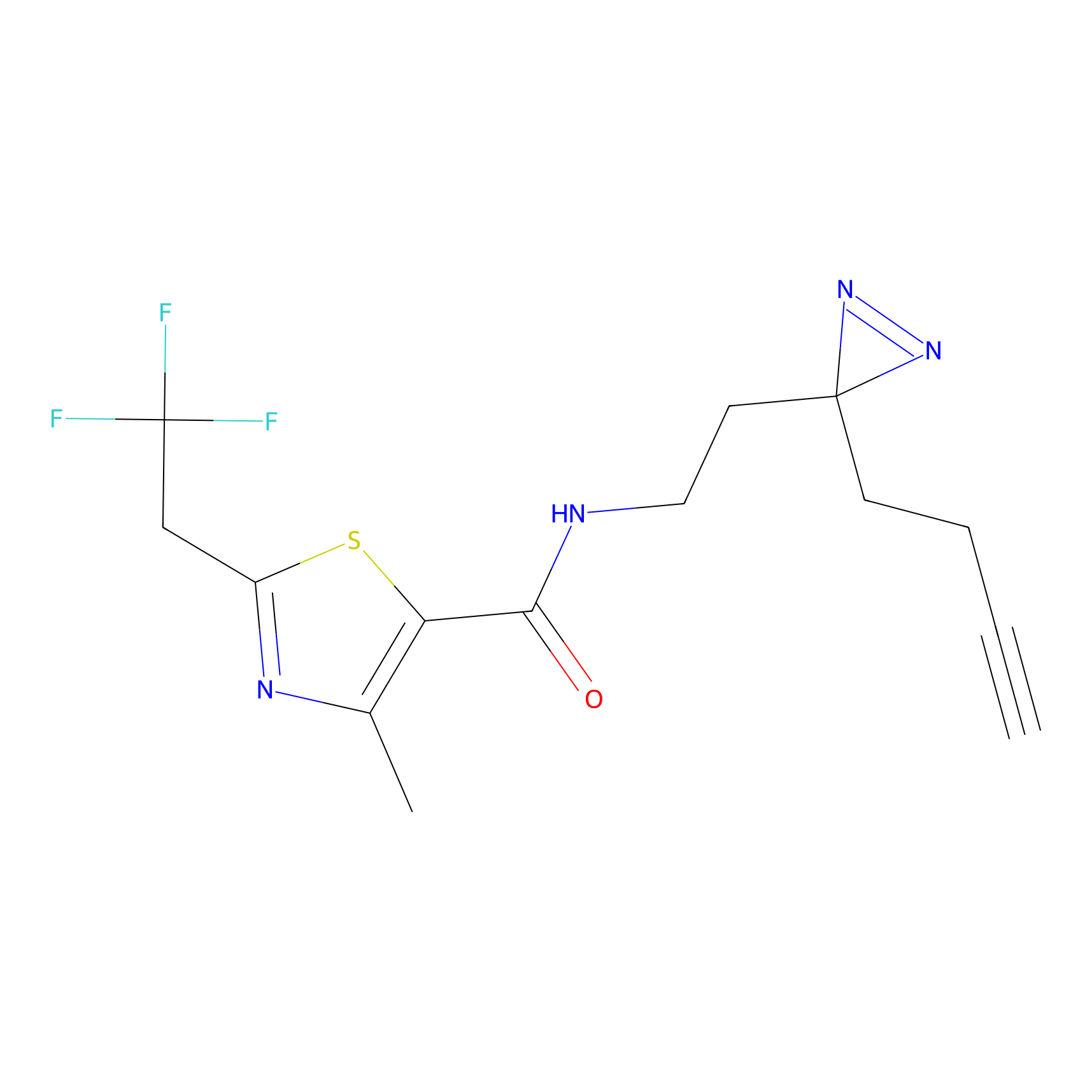
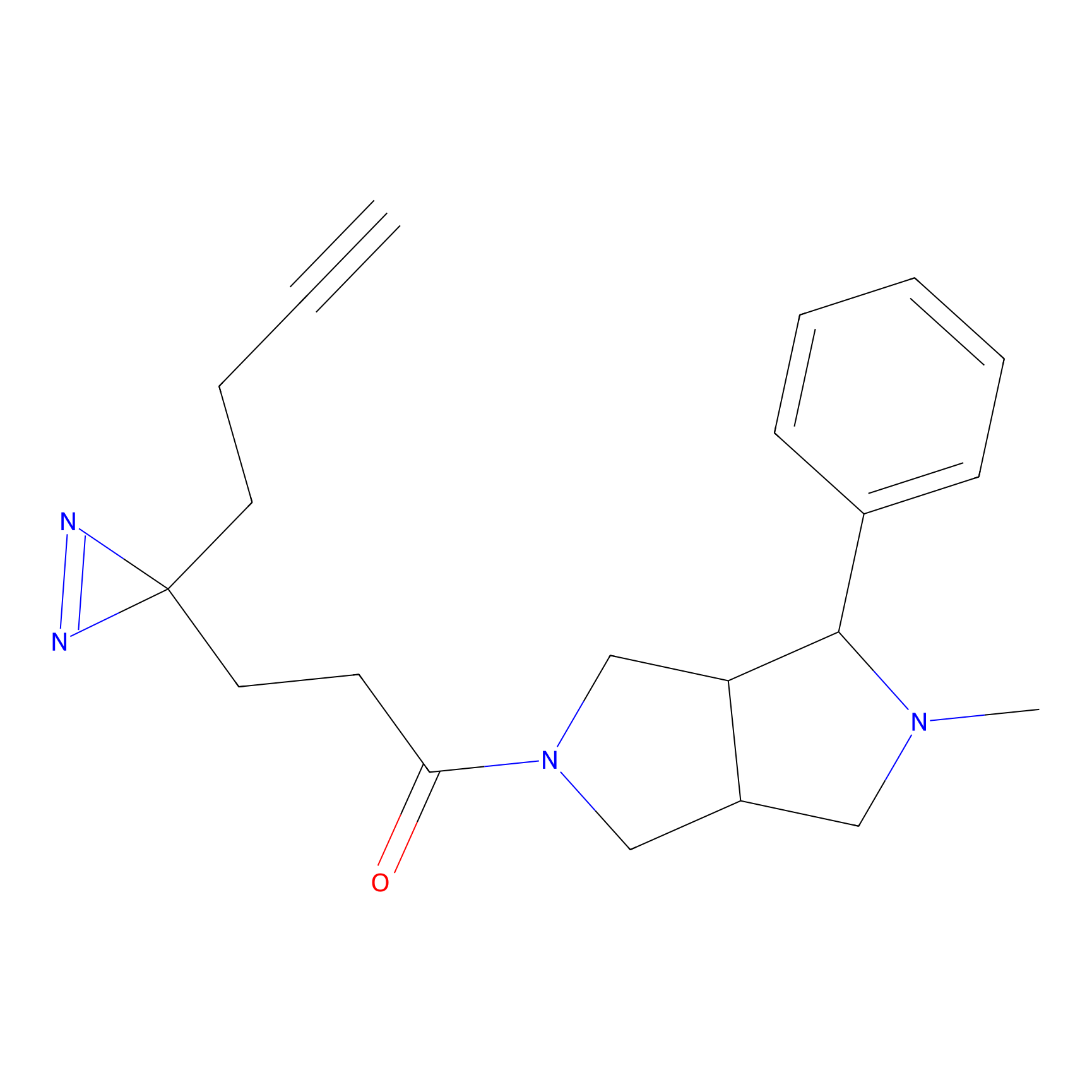
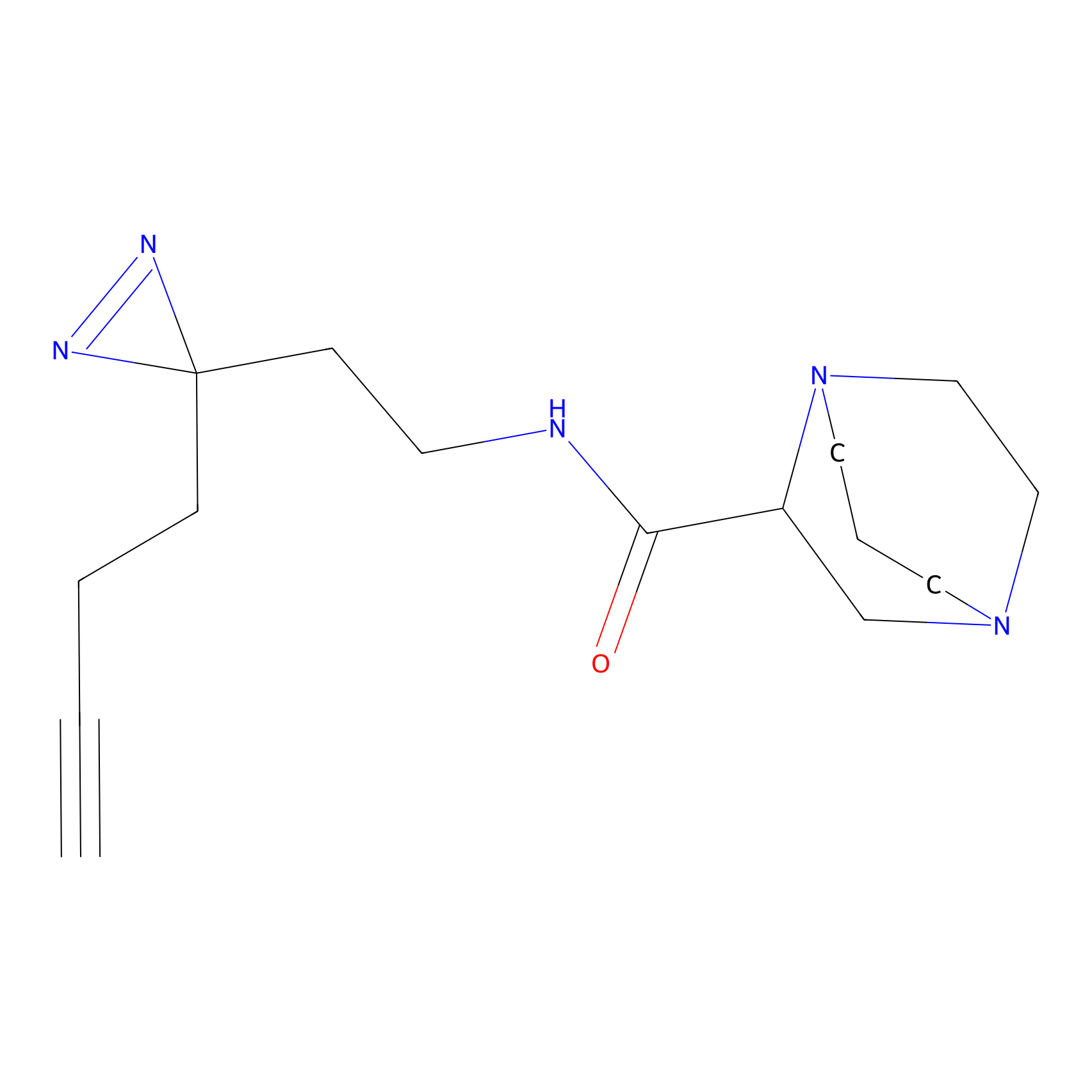
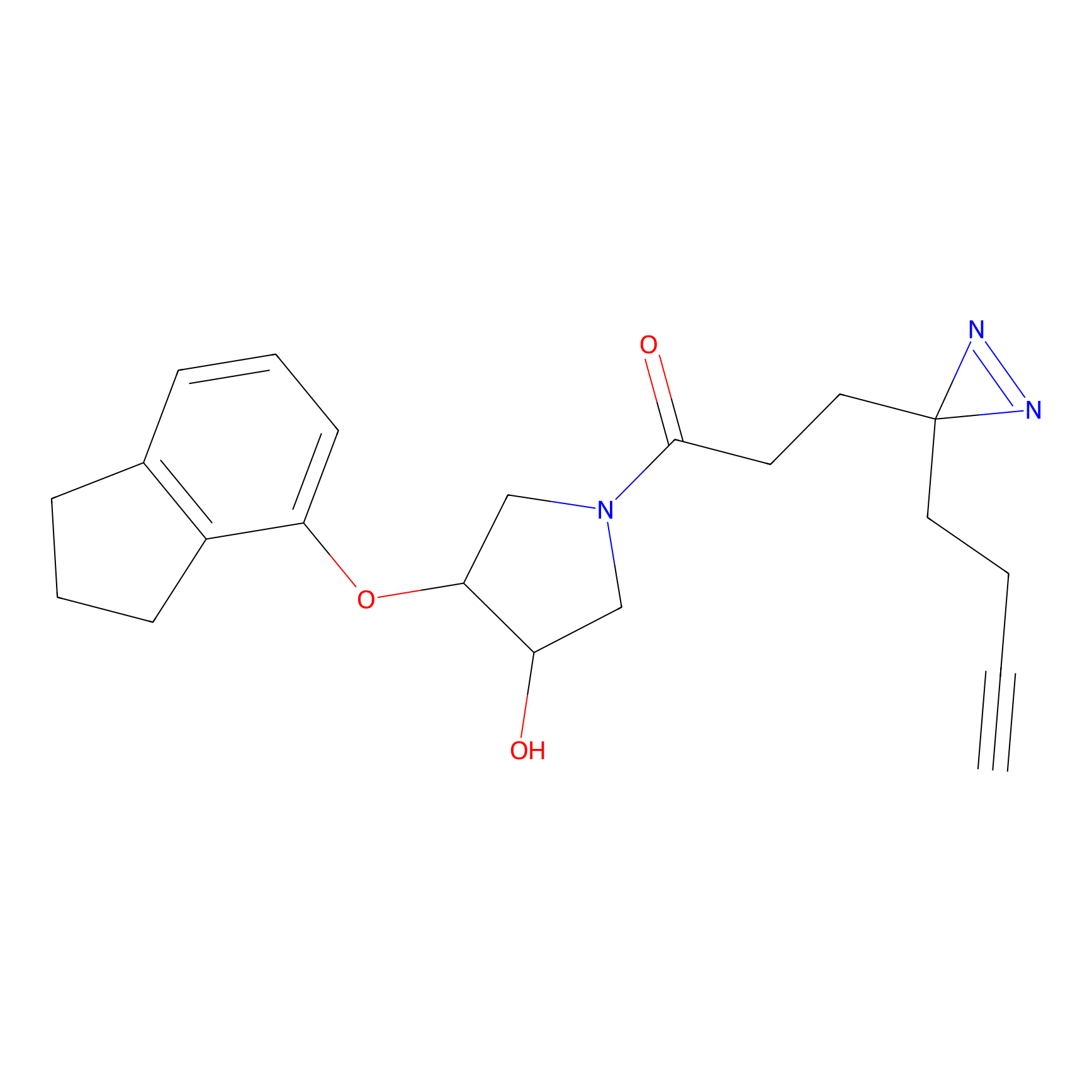
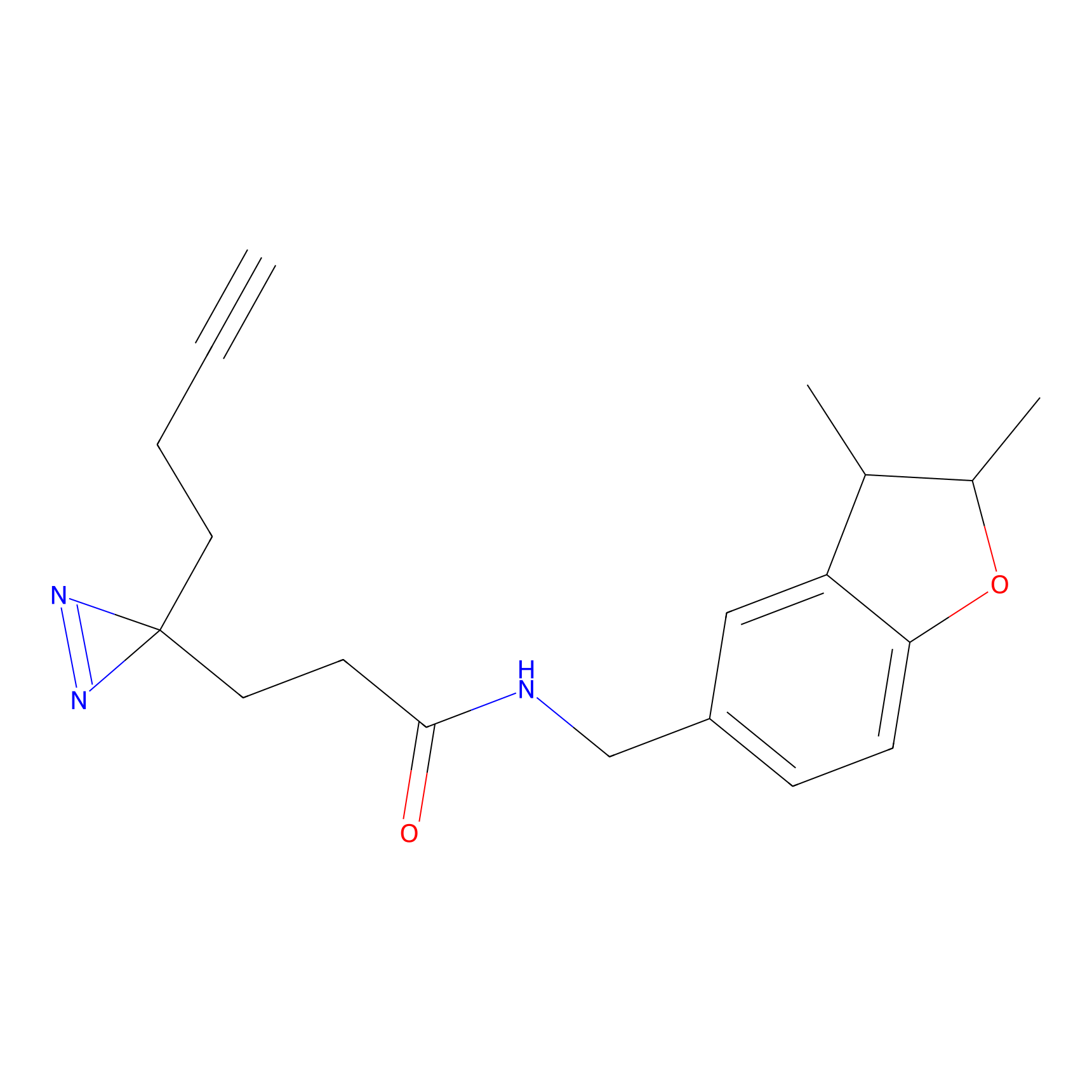
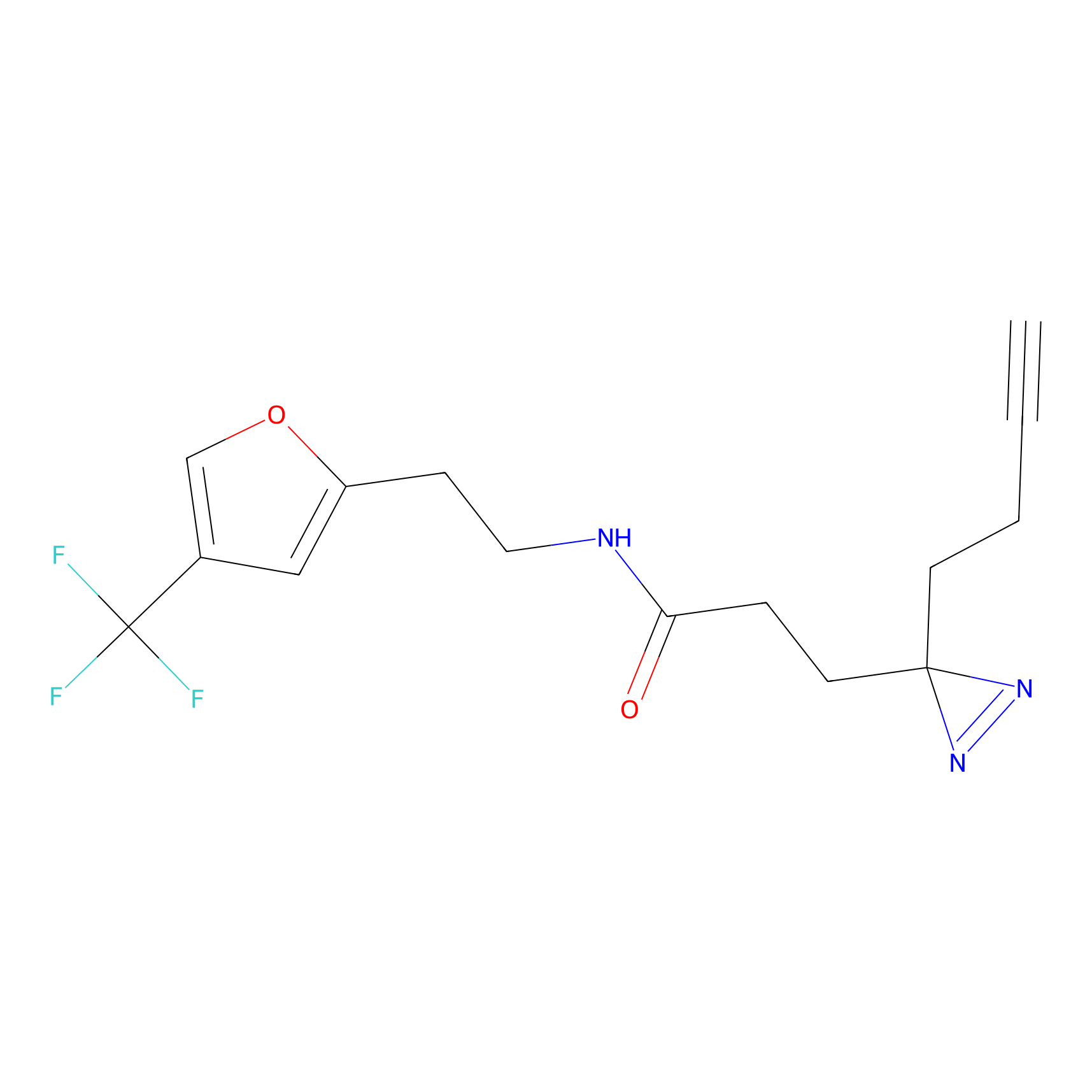
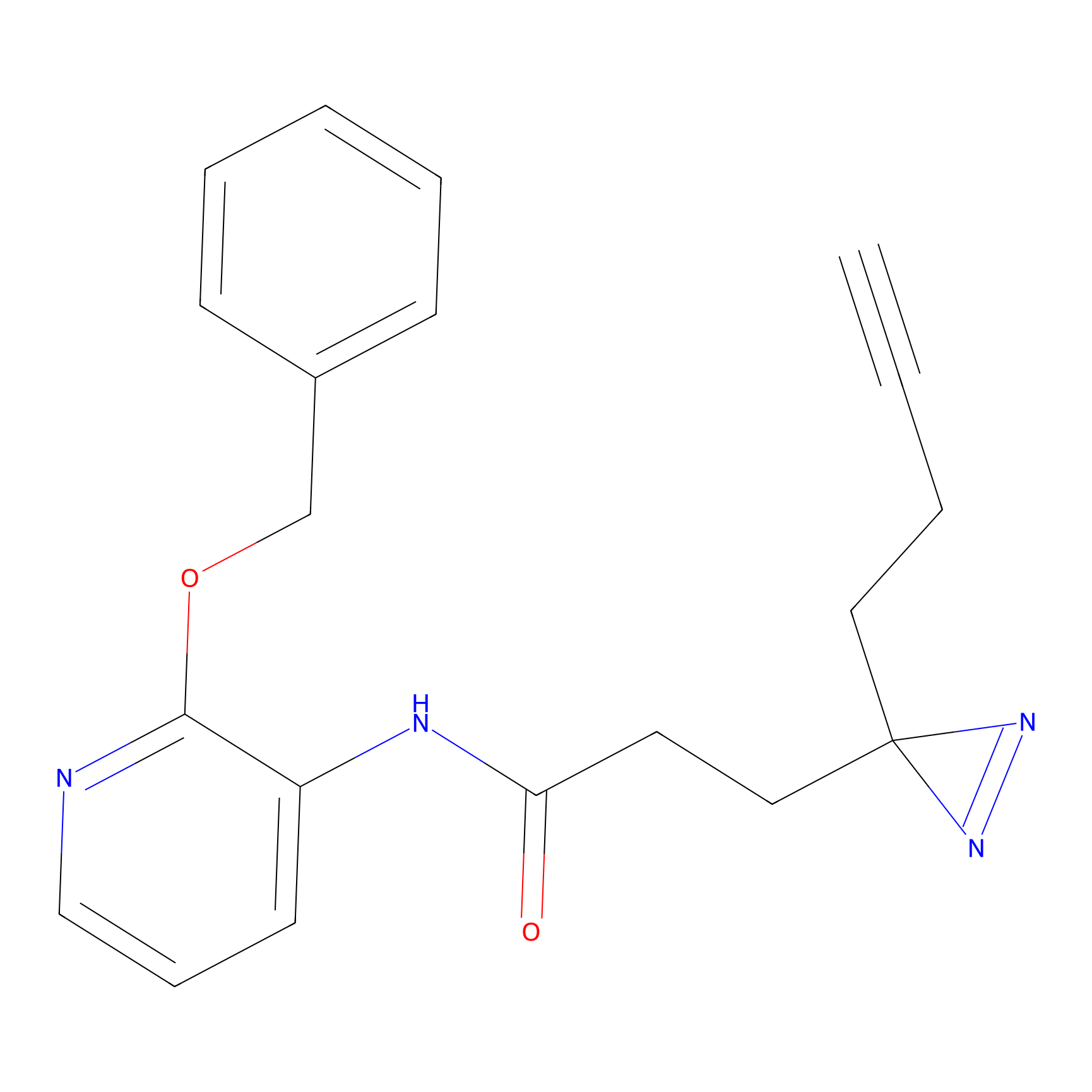
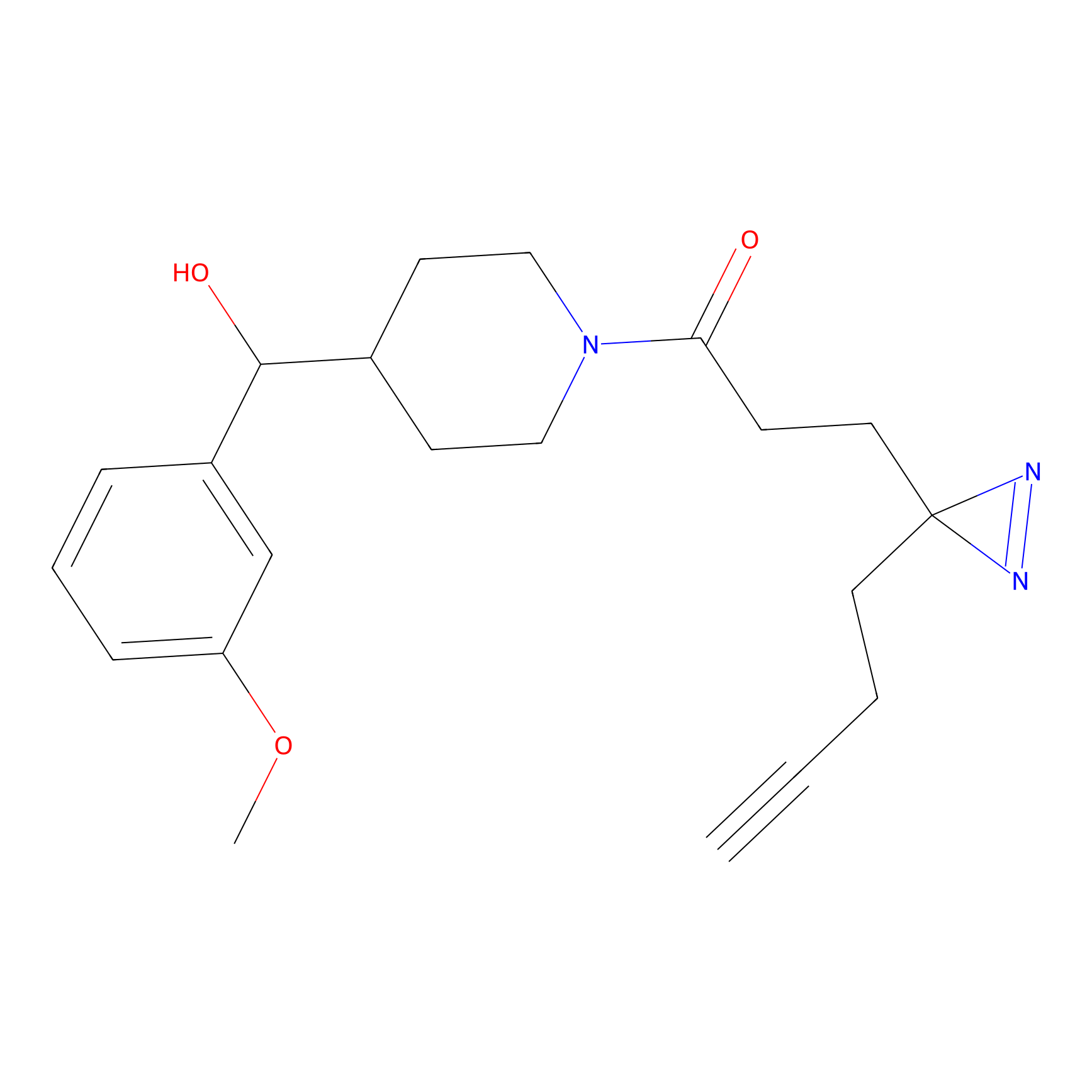
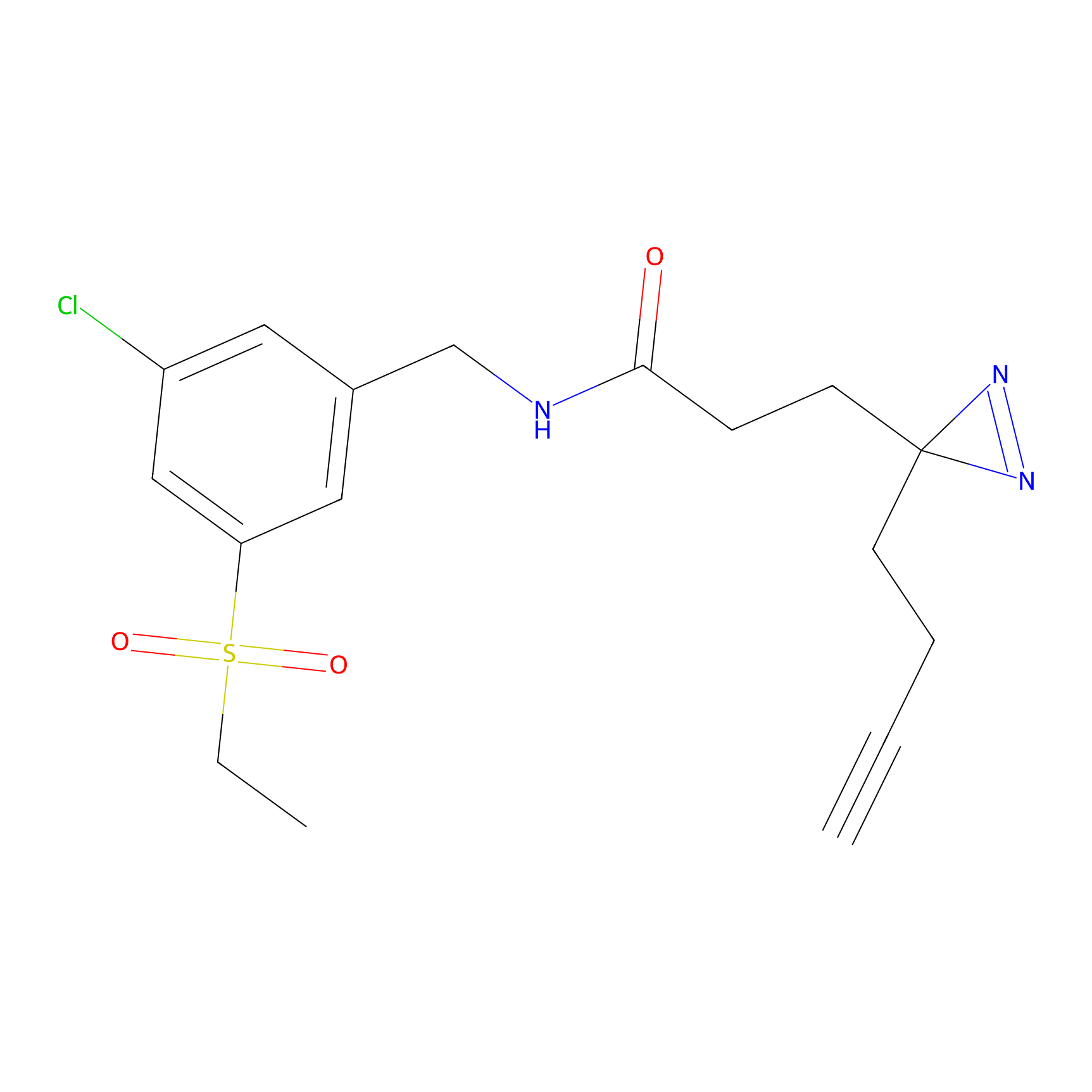
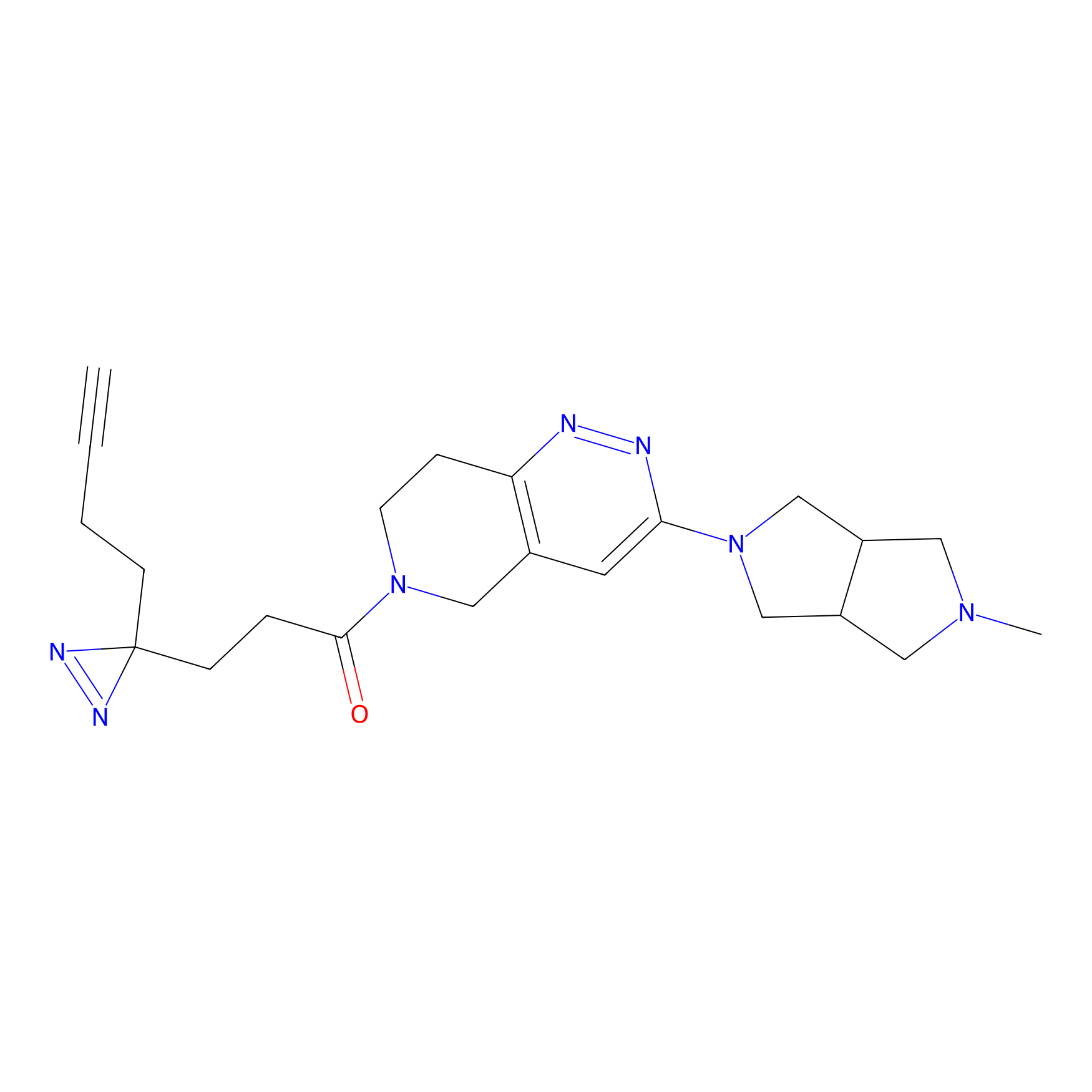
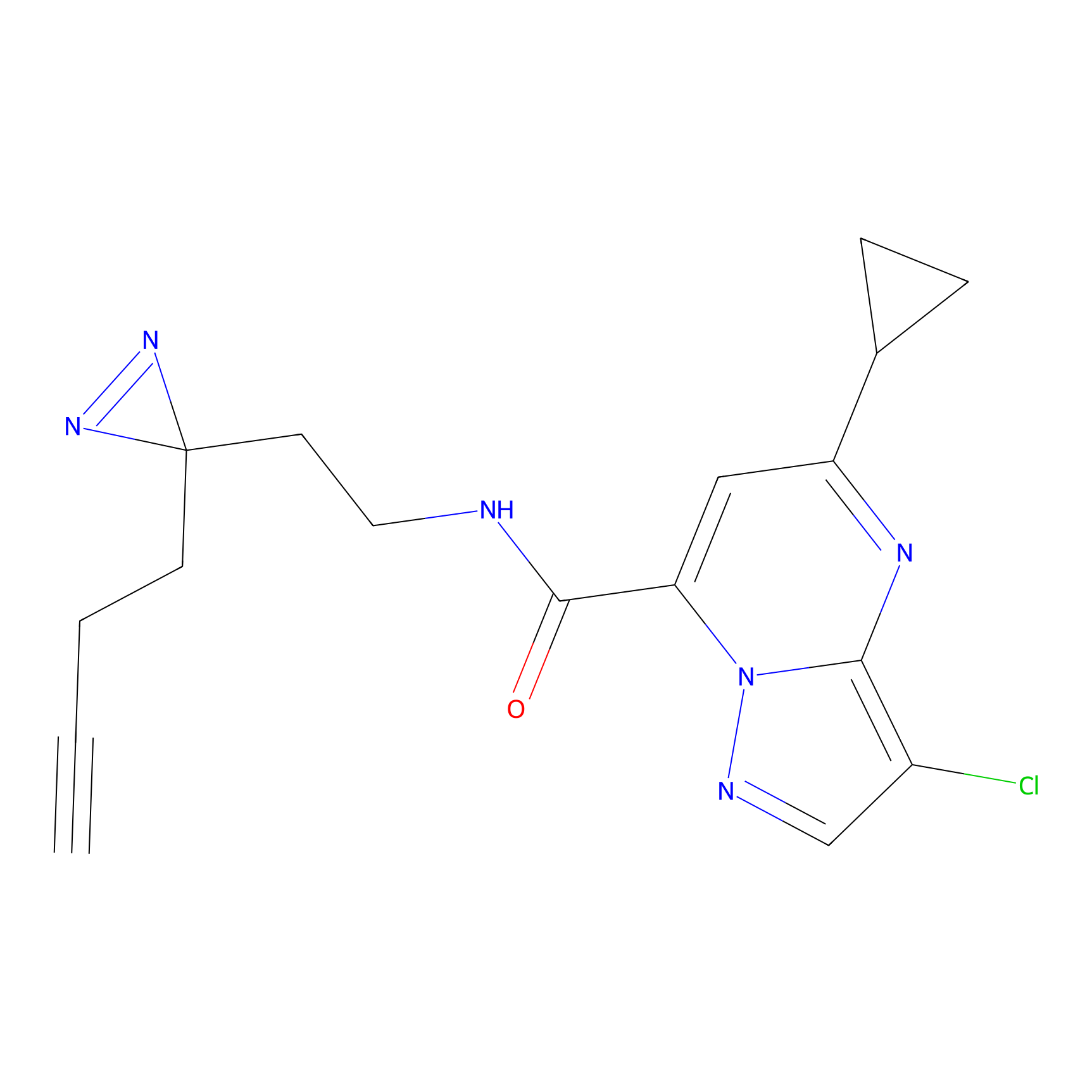
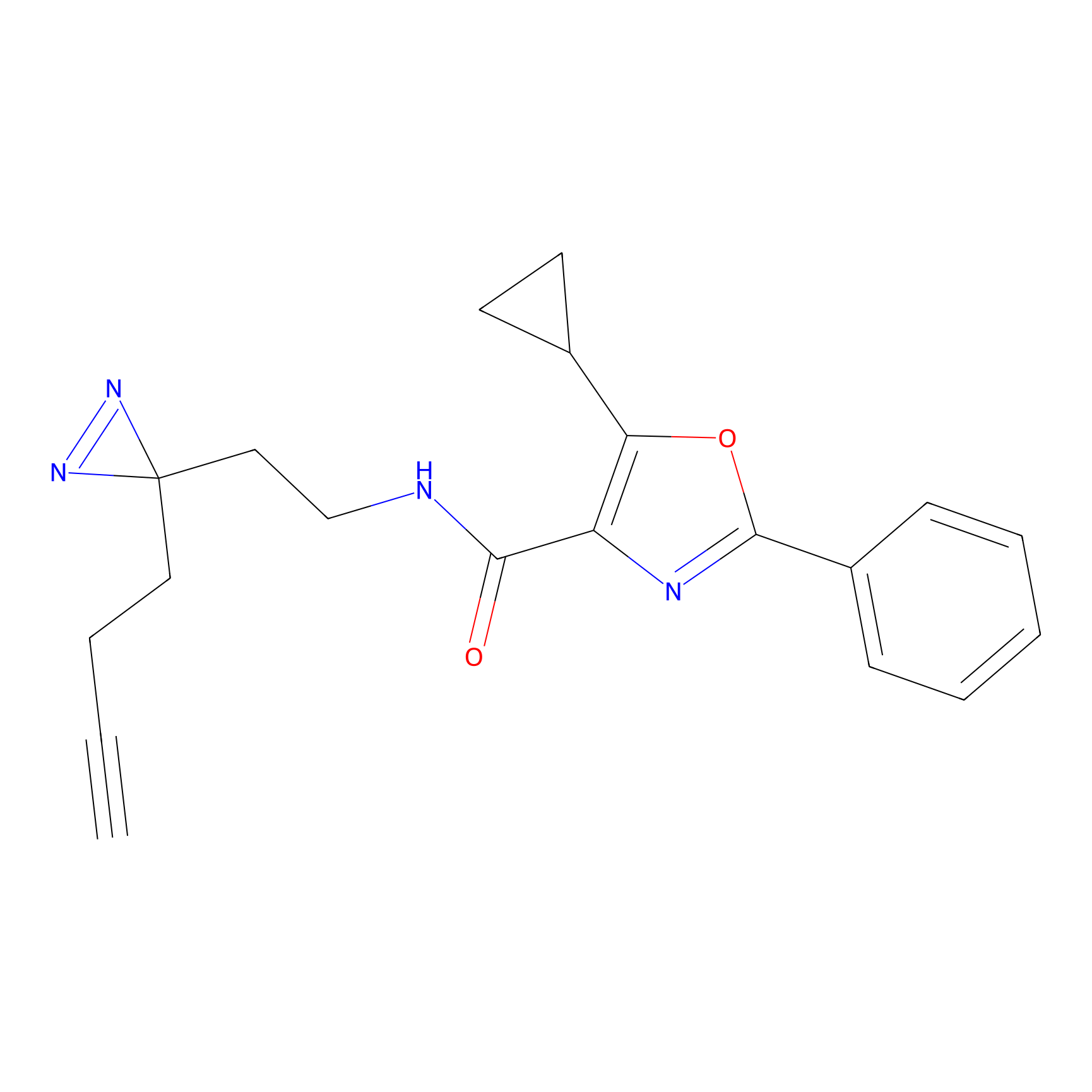
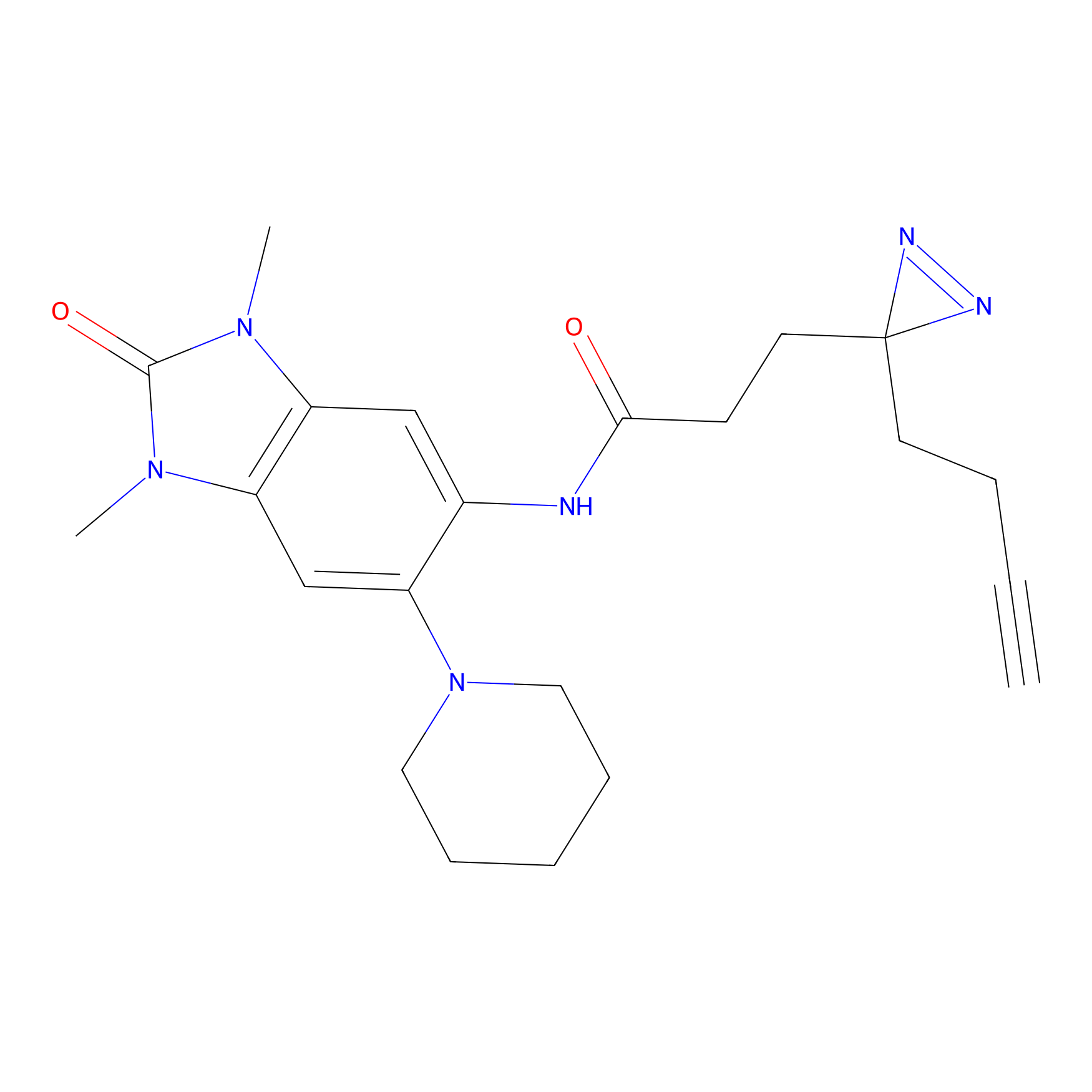
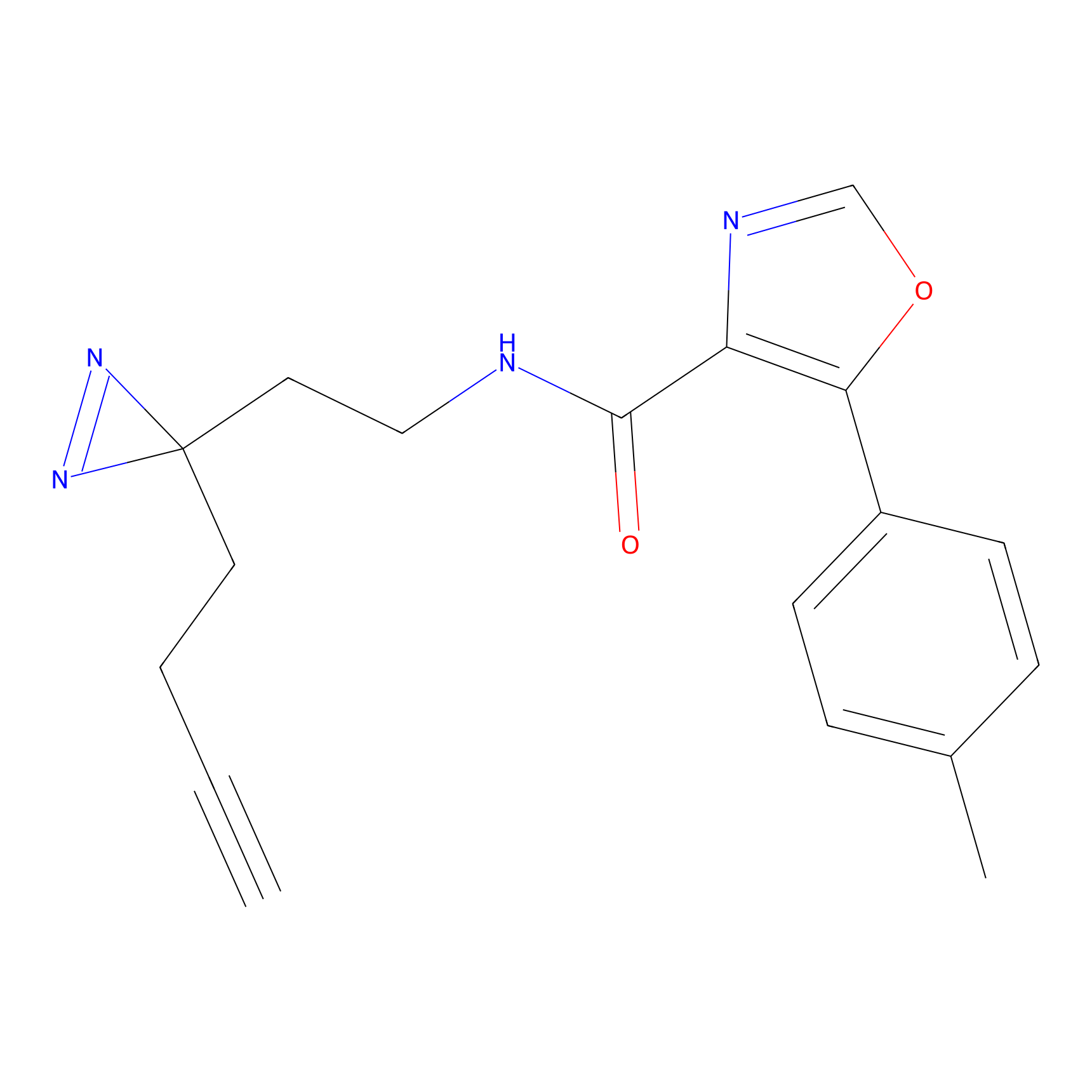
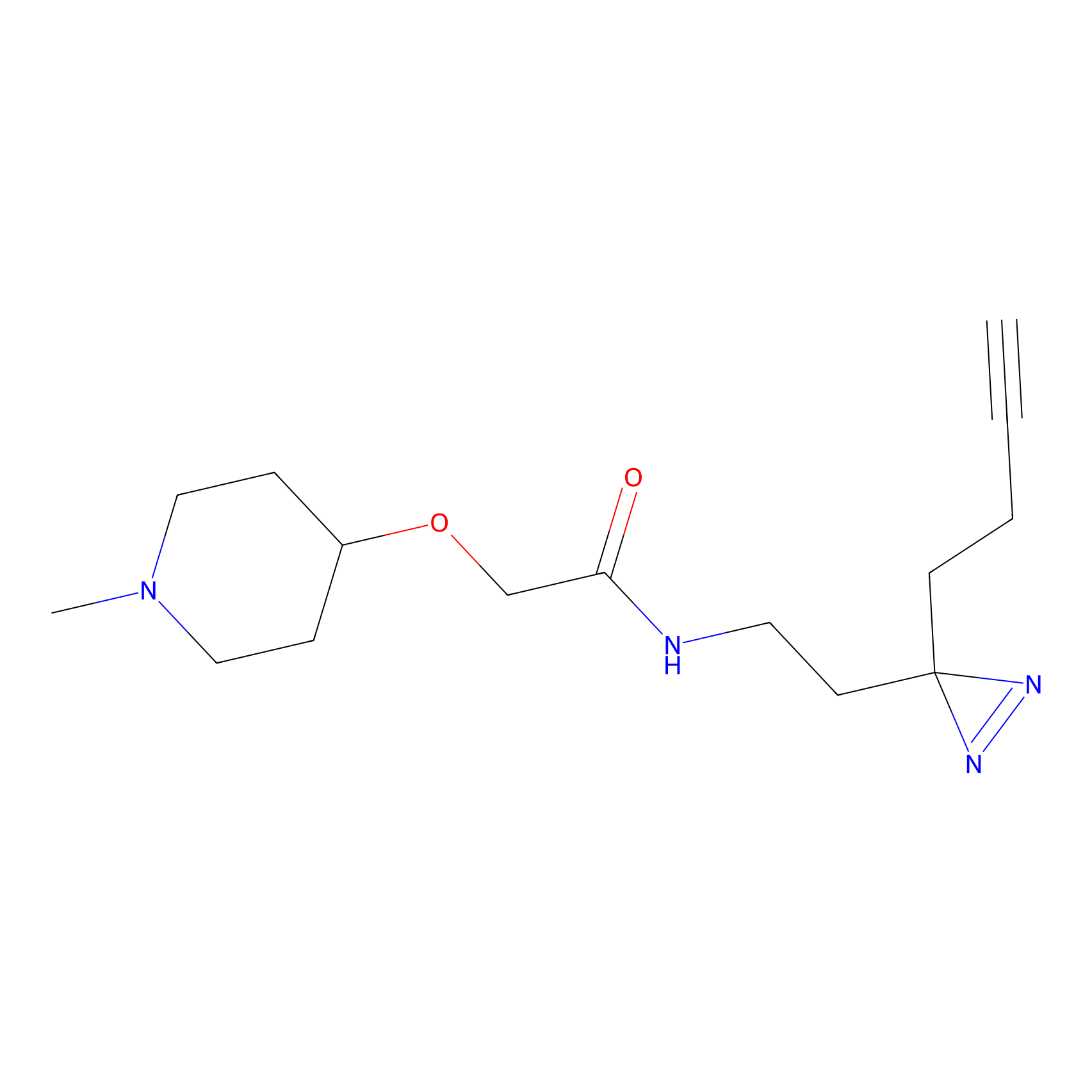
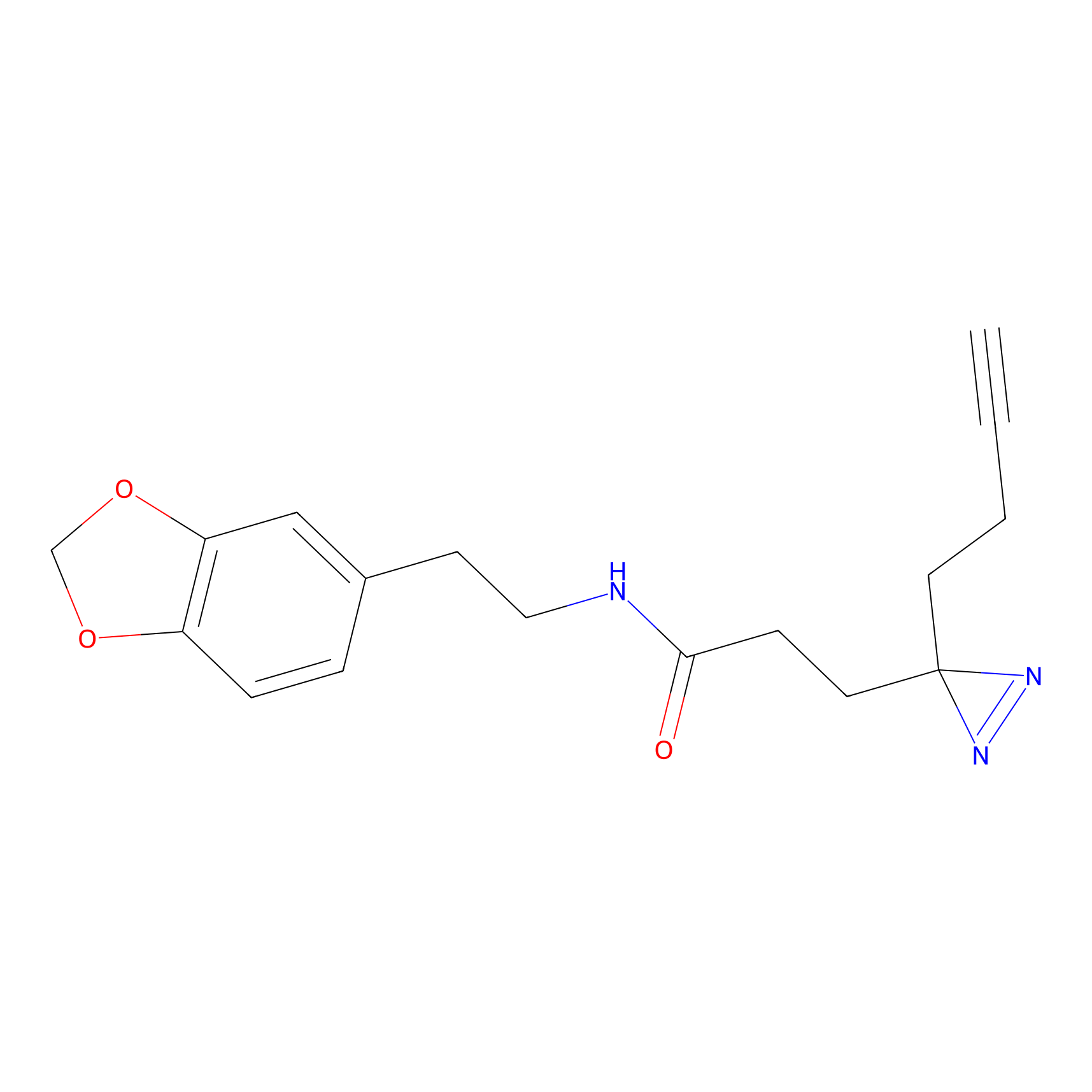
HDSF-alk Probe Info |
 |
3.57 | LDD0197 | [1] | |
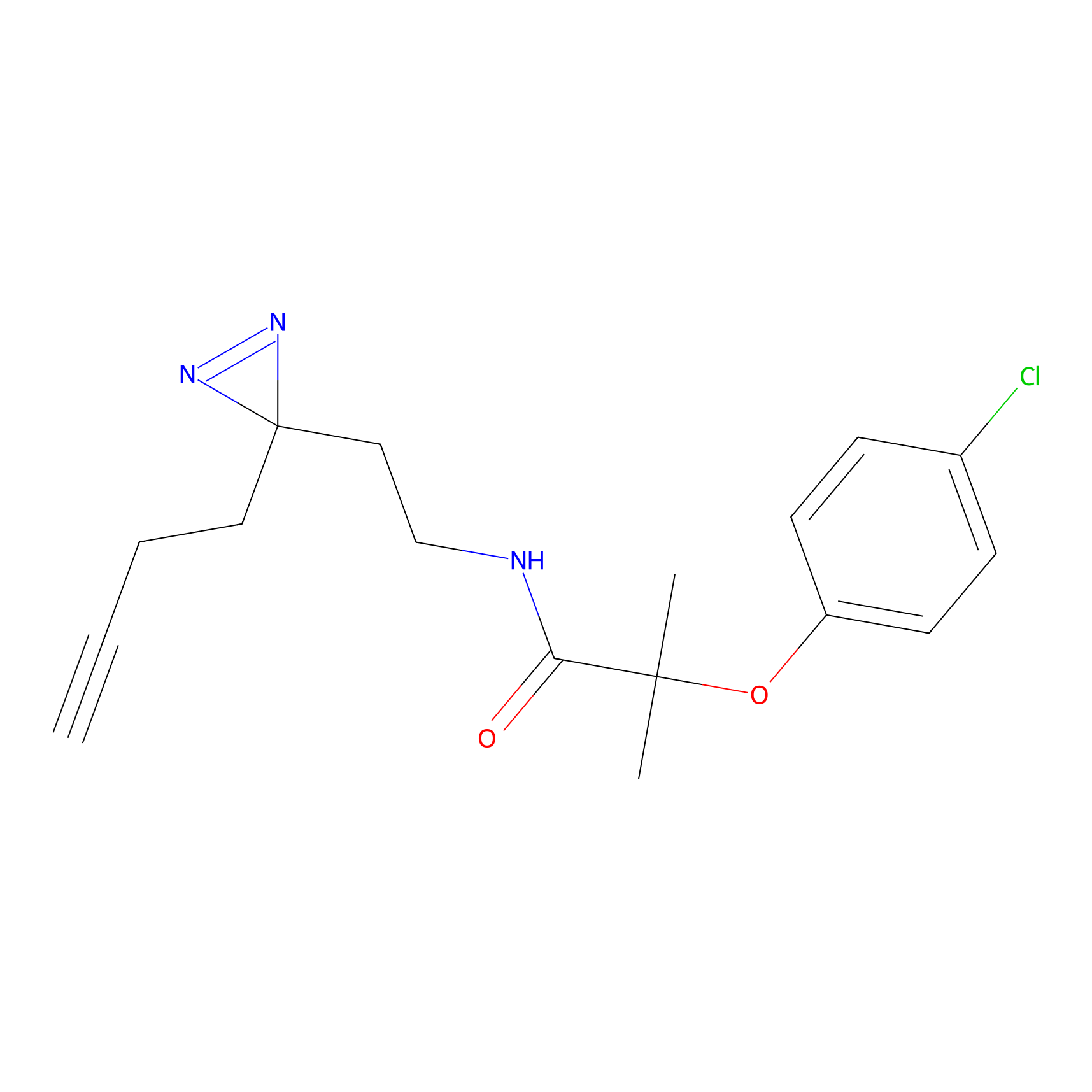
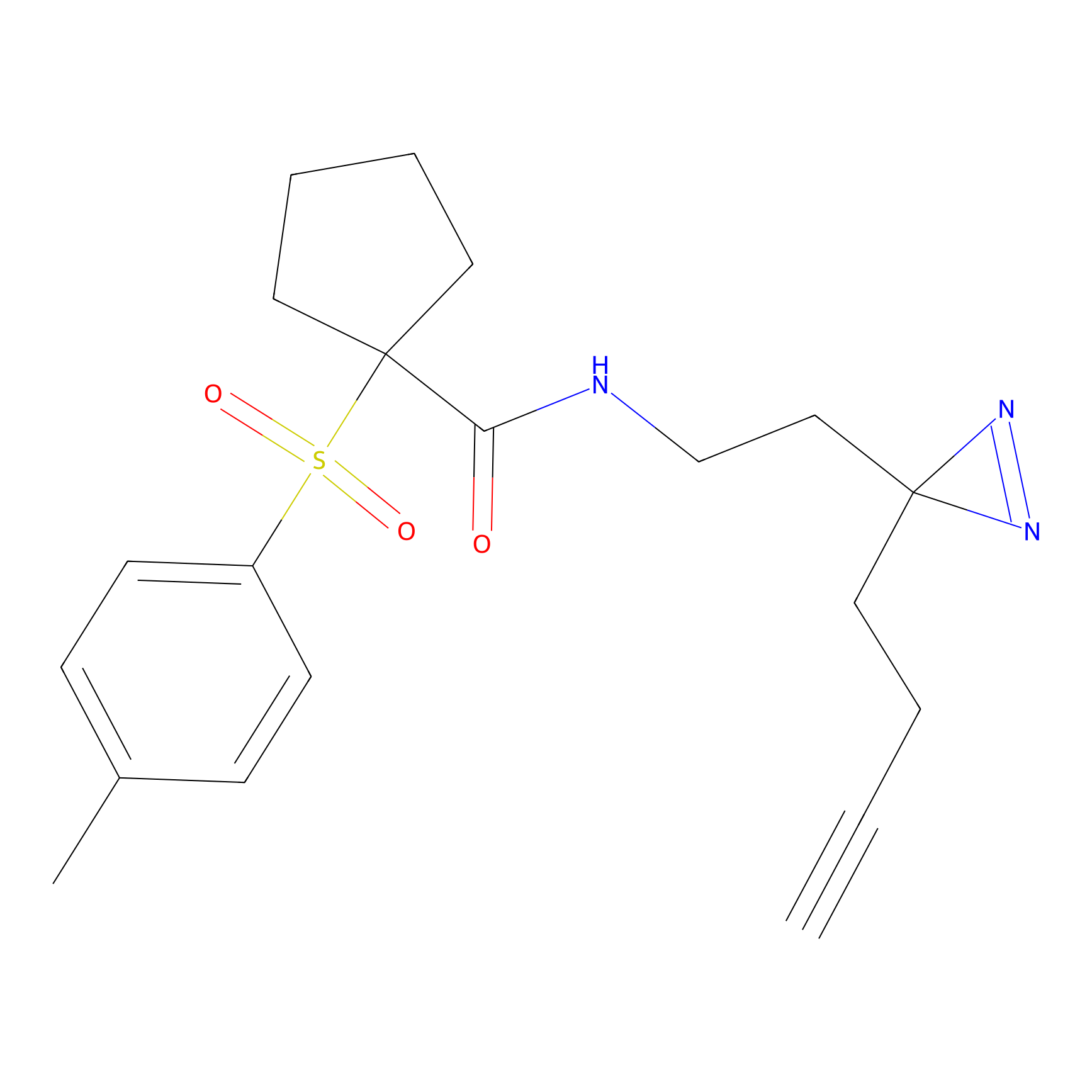
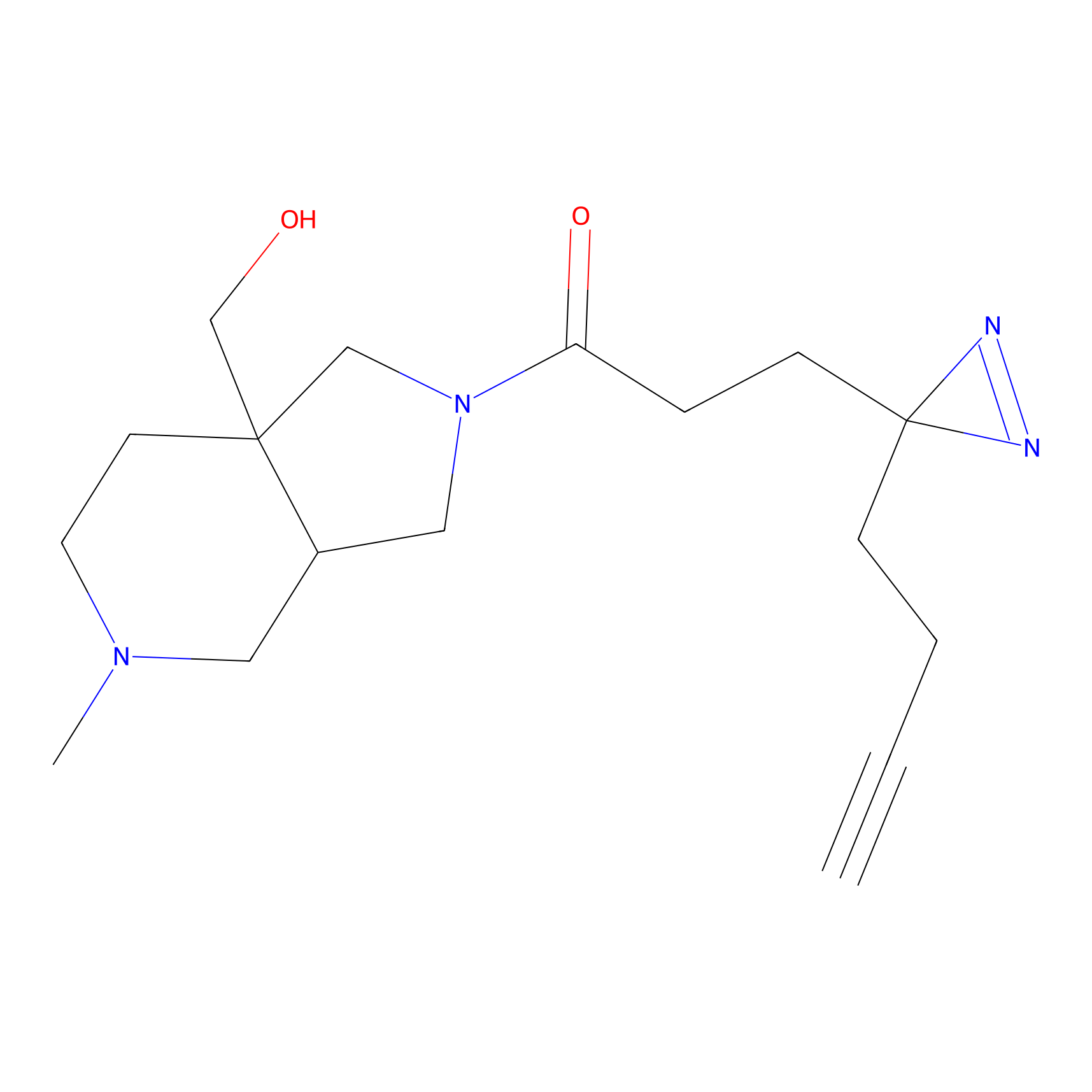
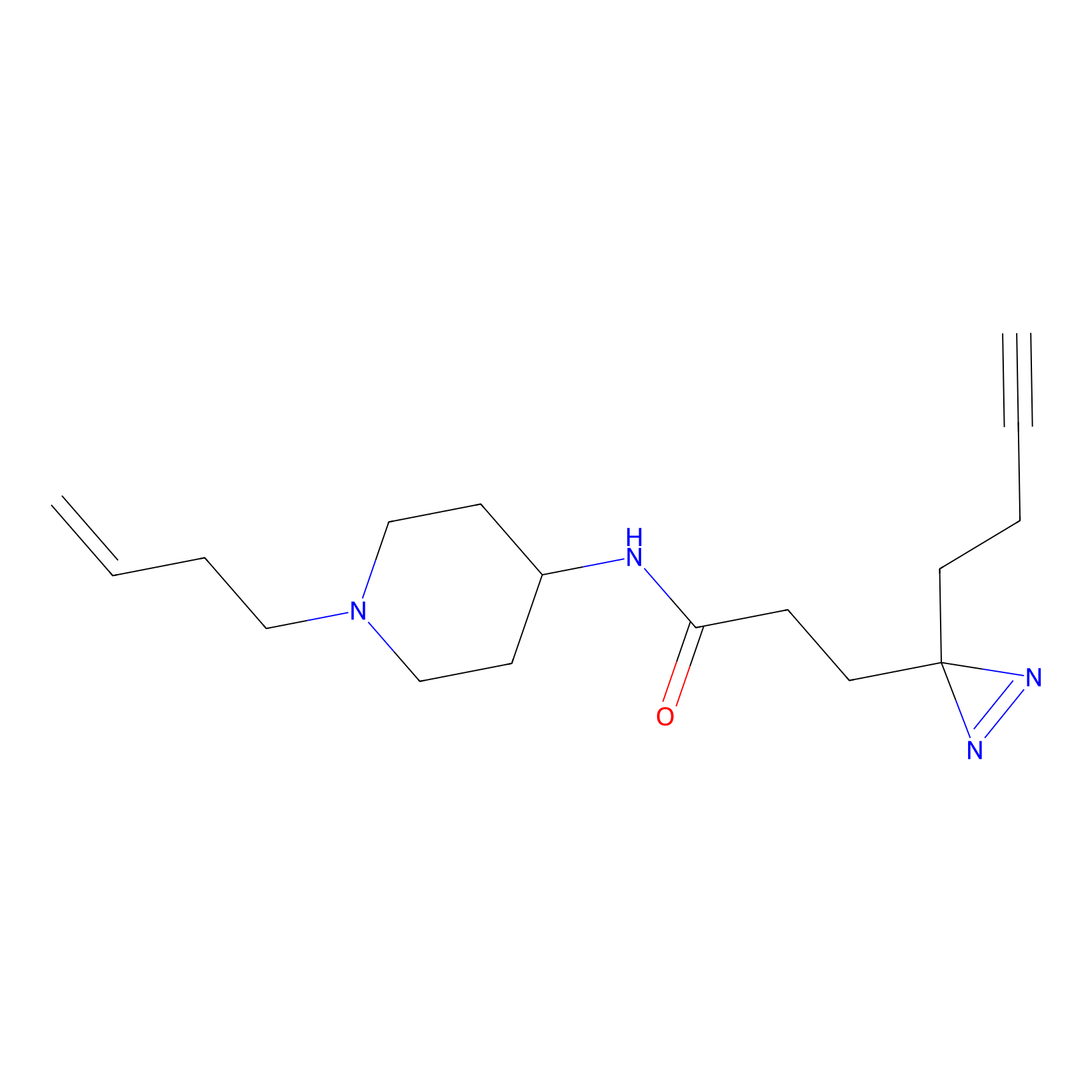
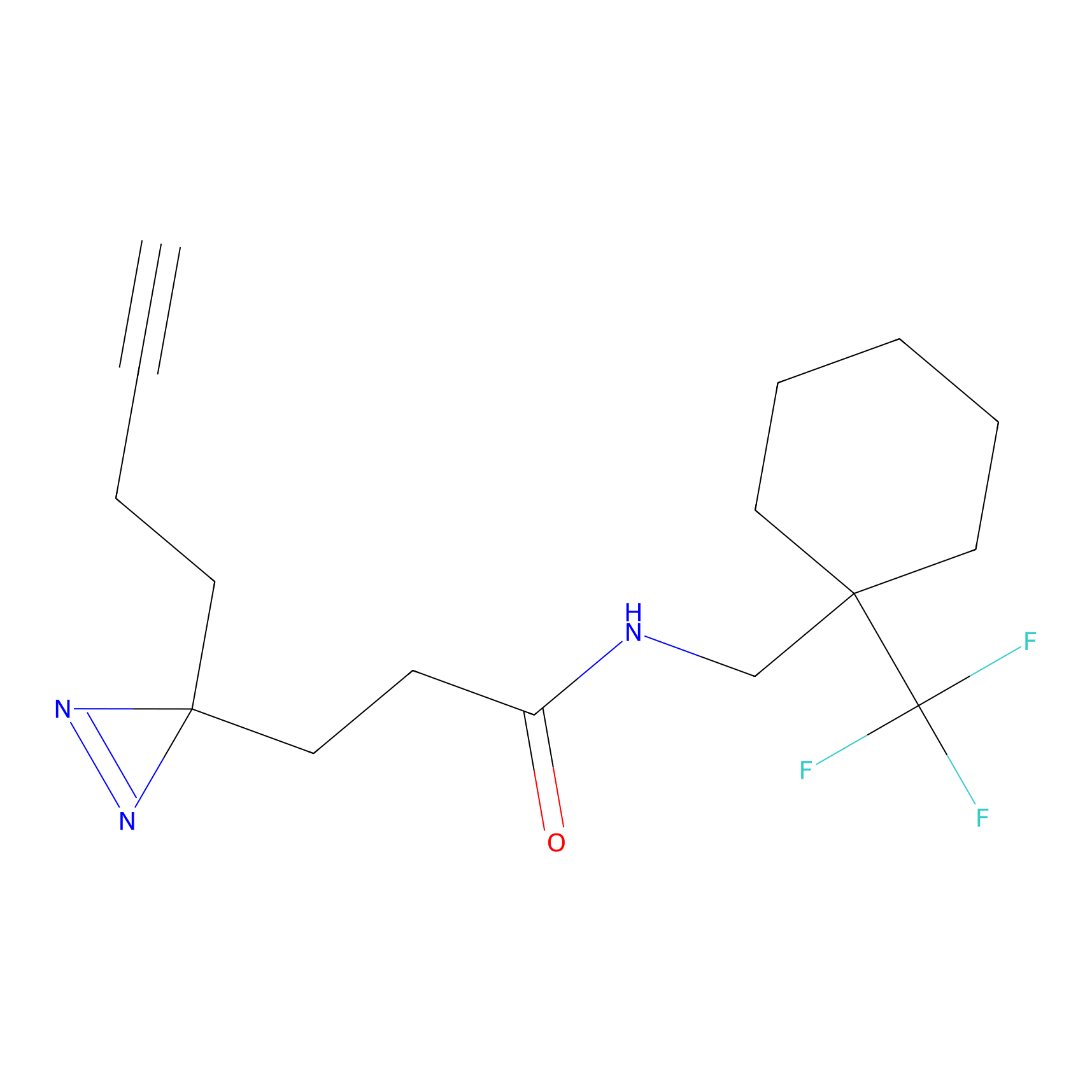
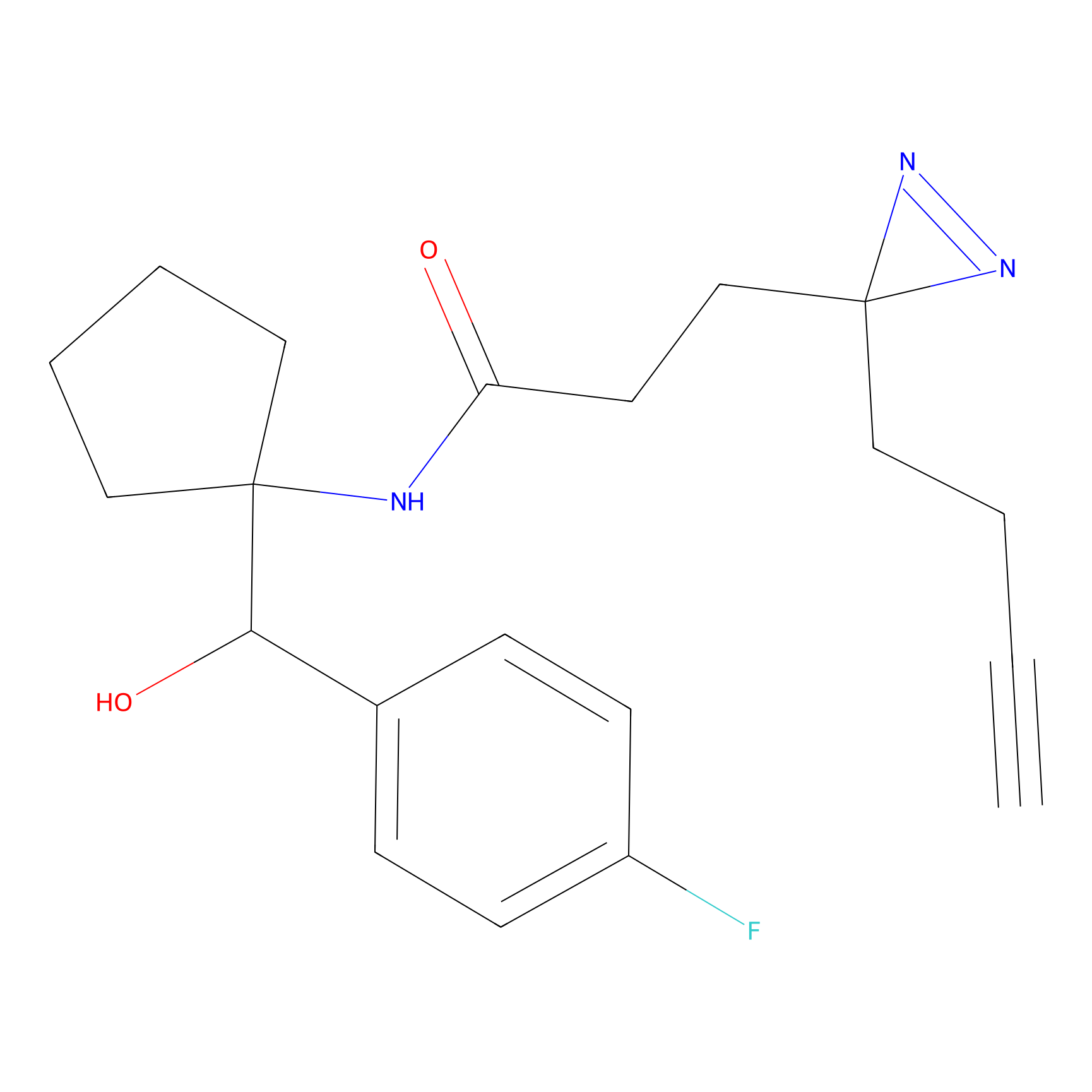
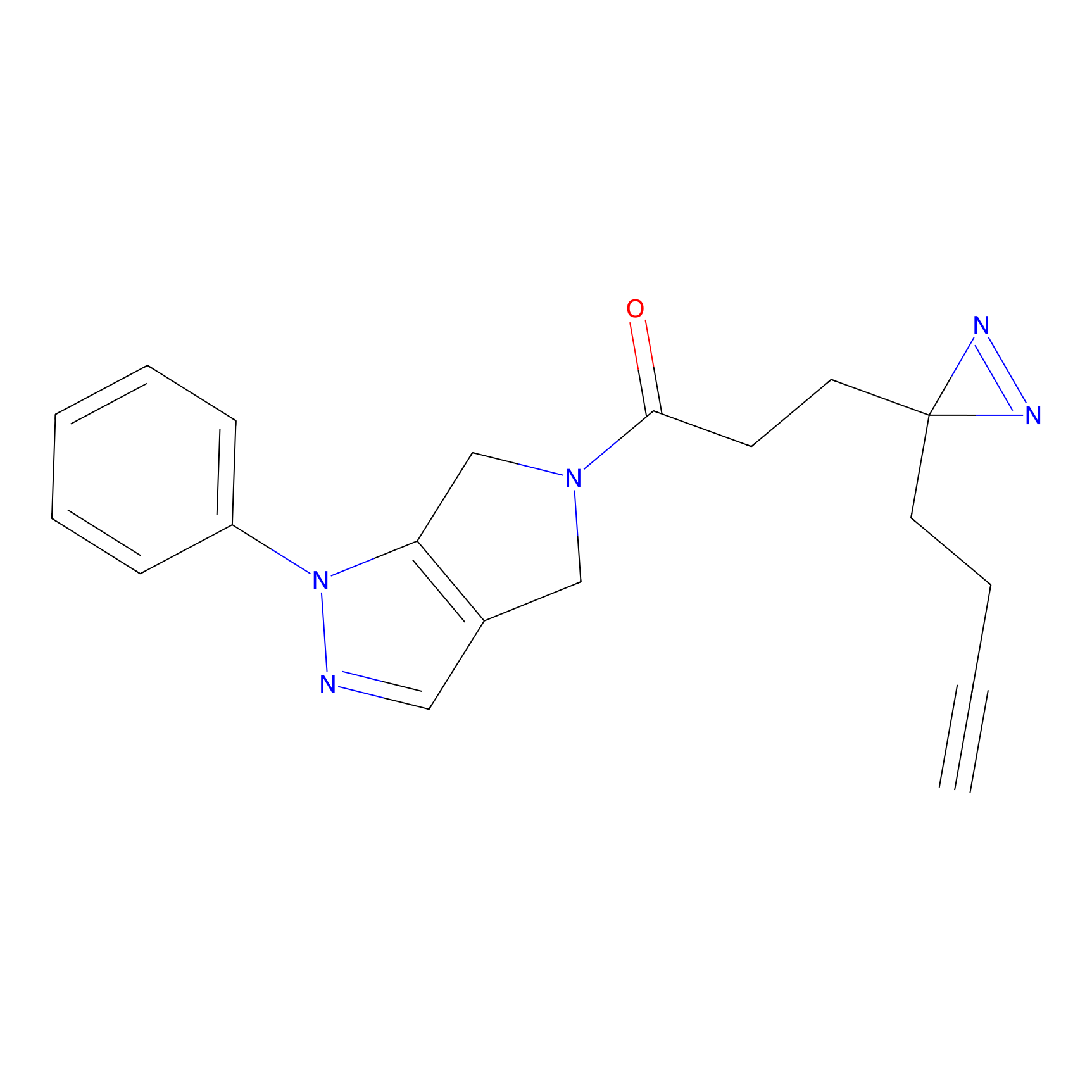
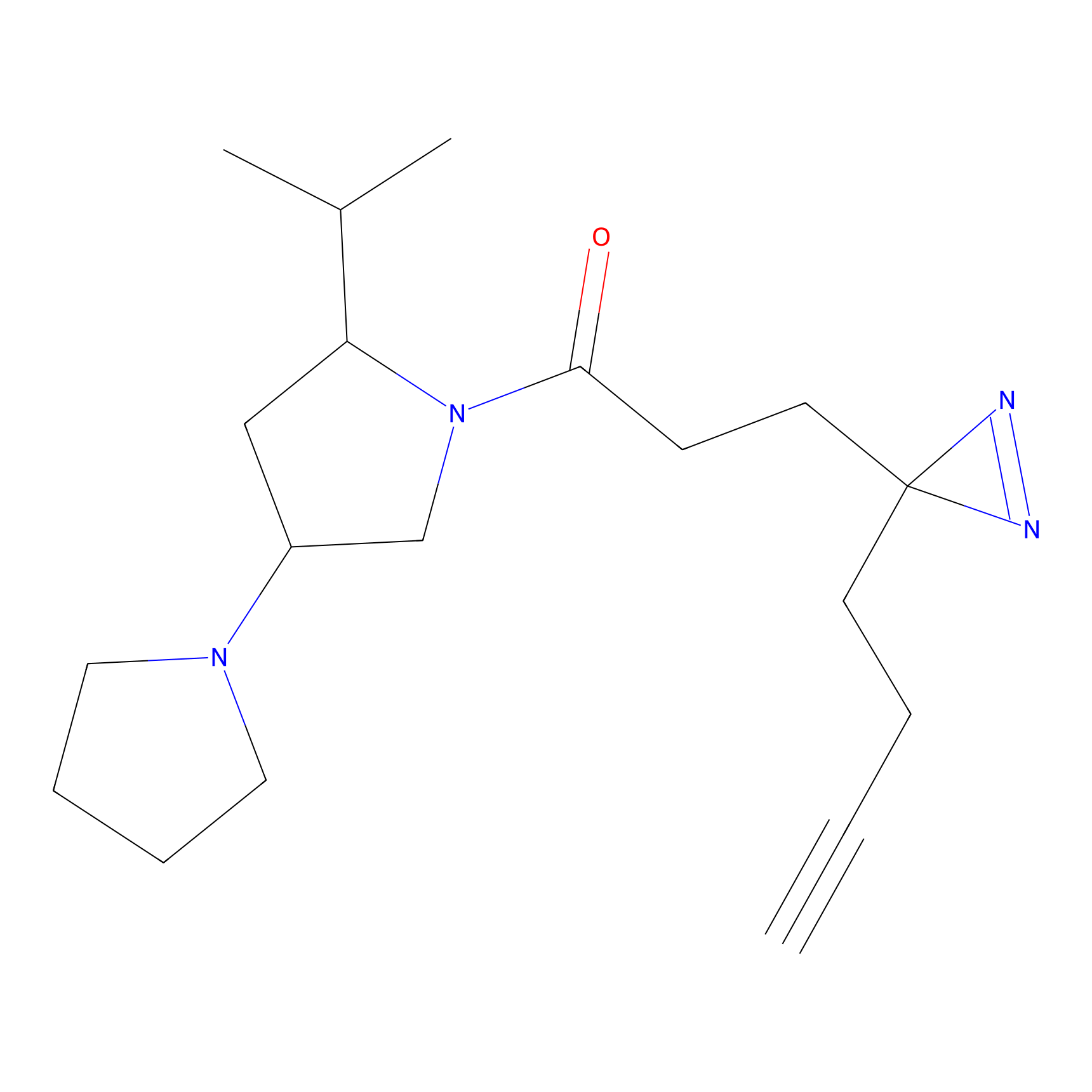
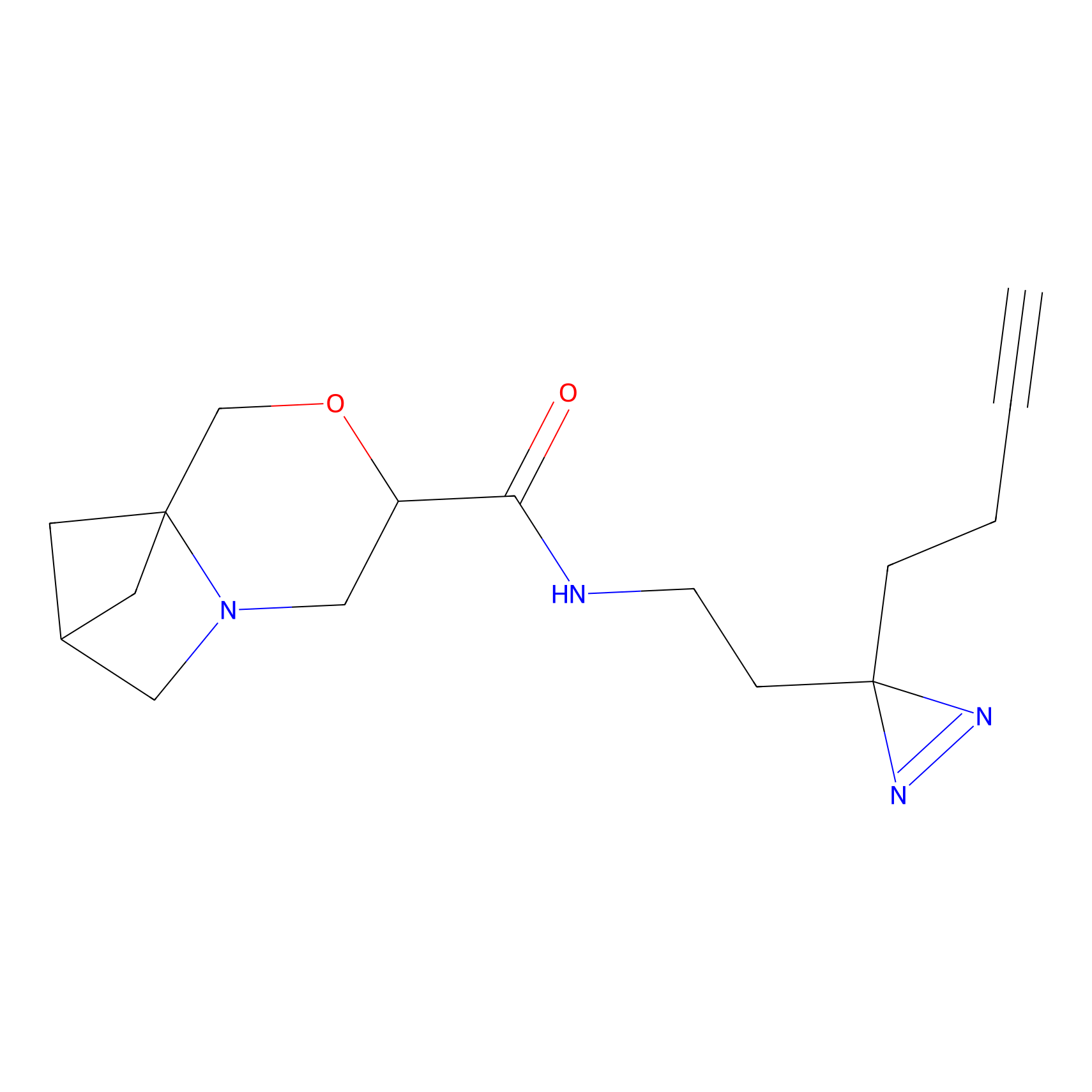
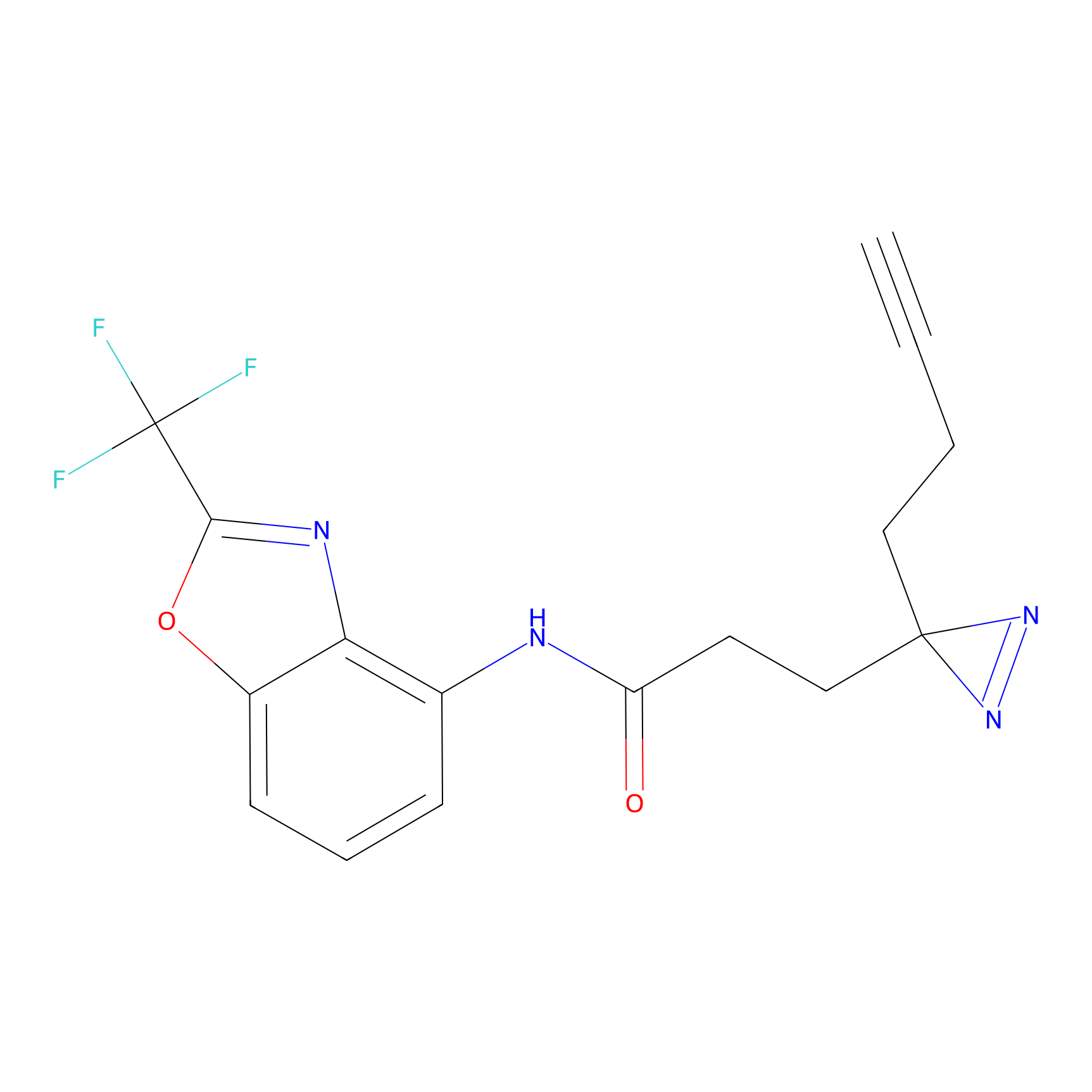
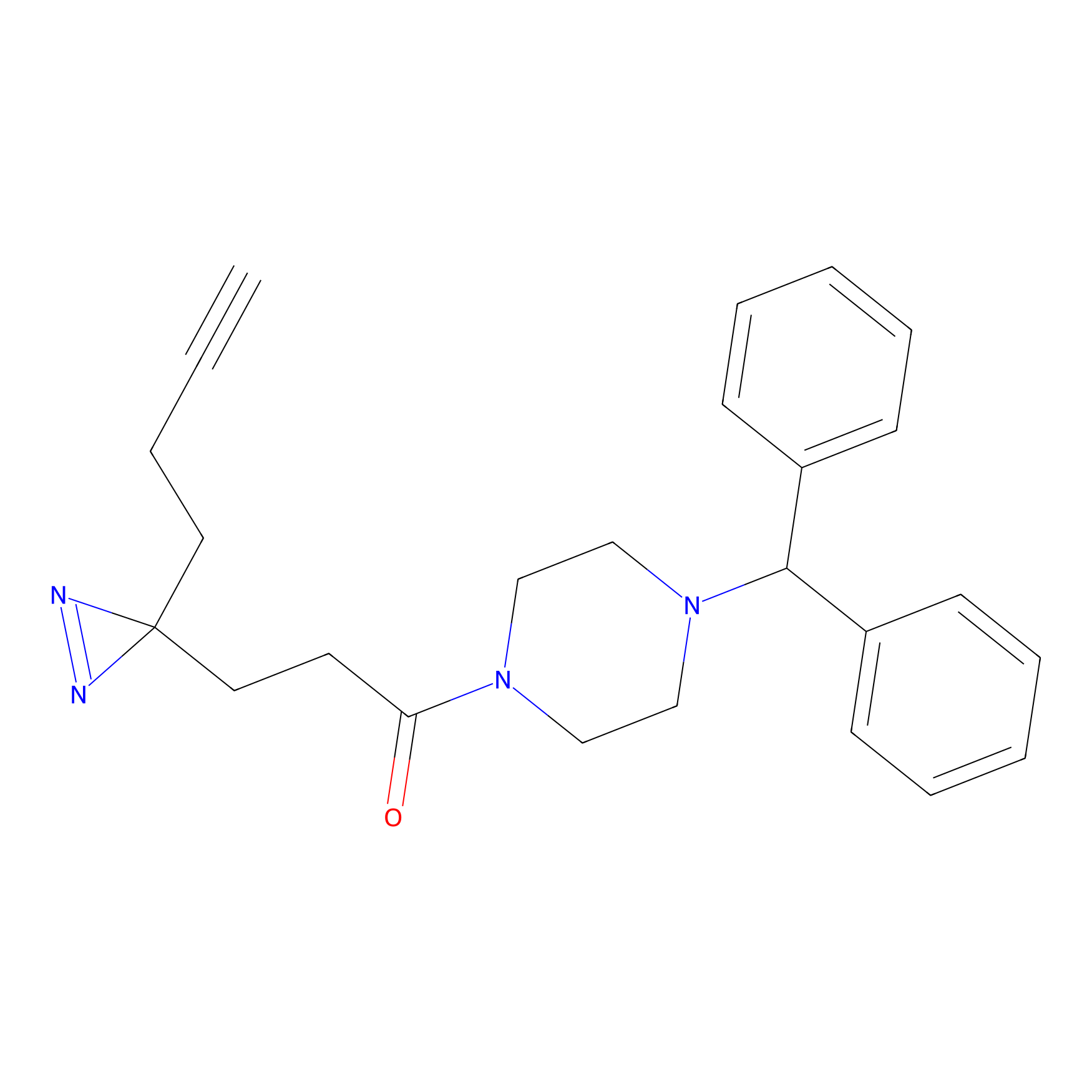
|
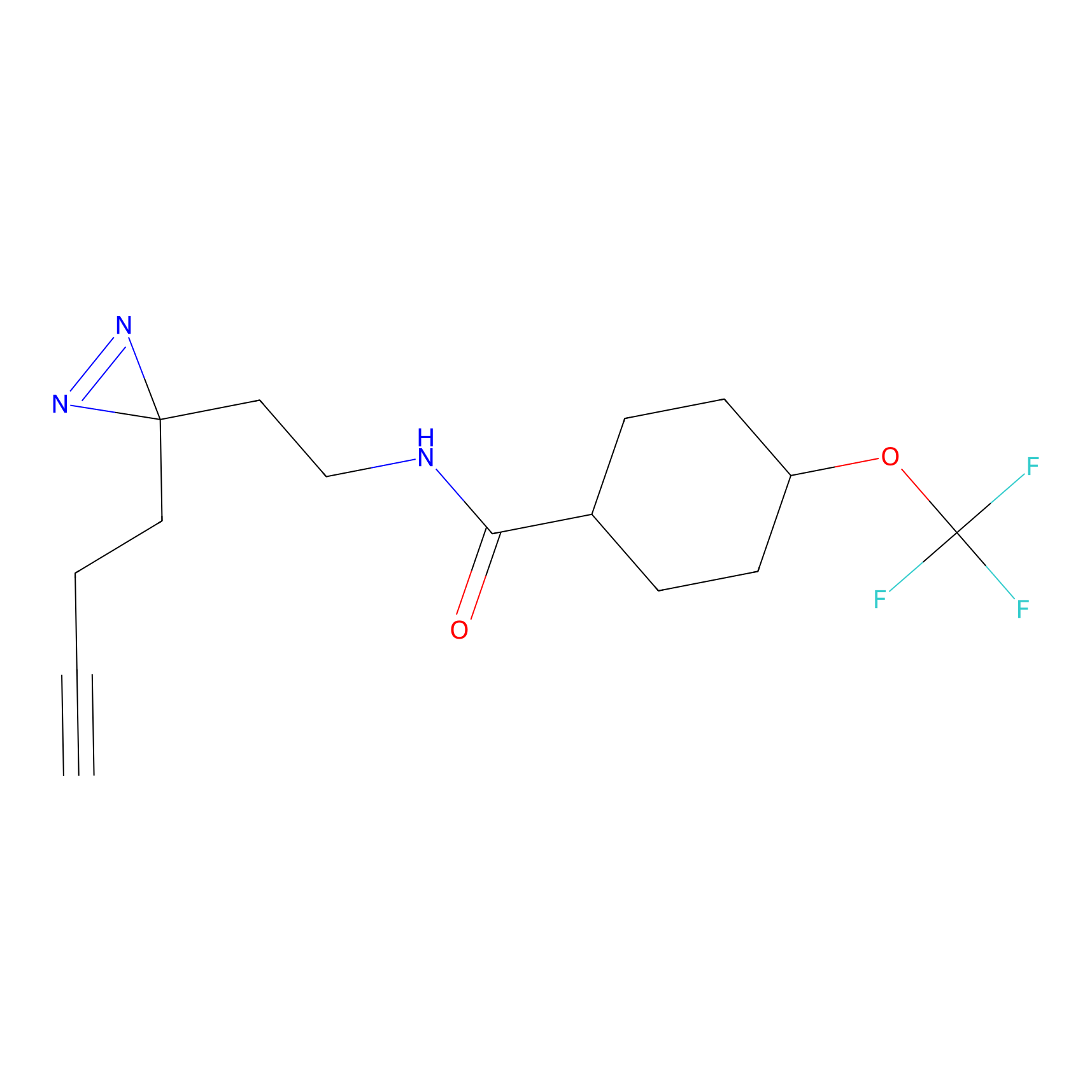
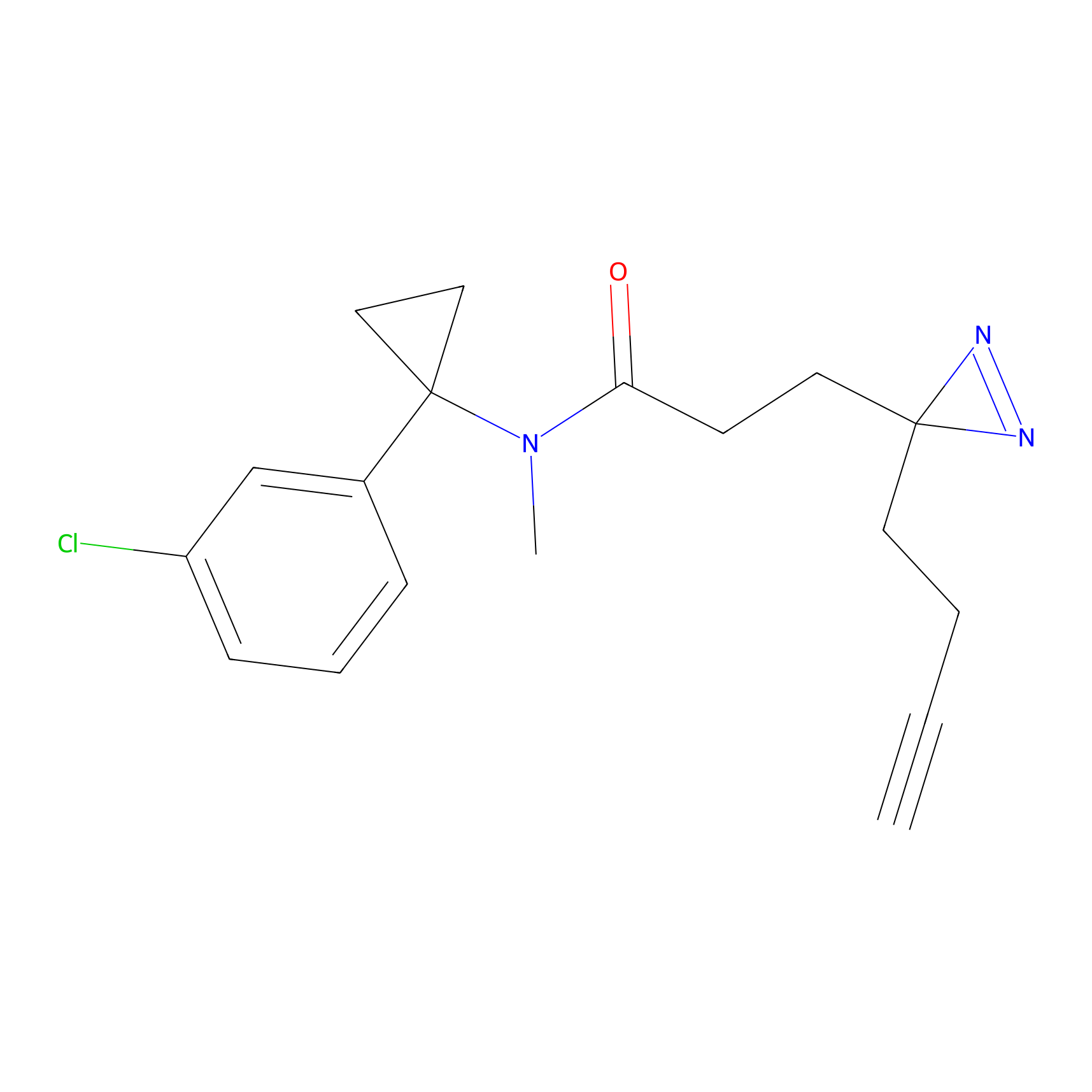
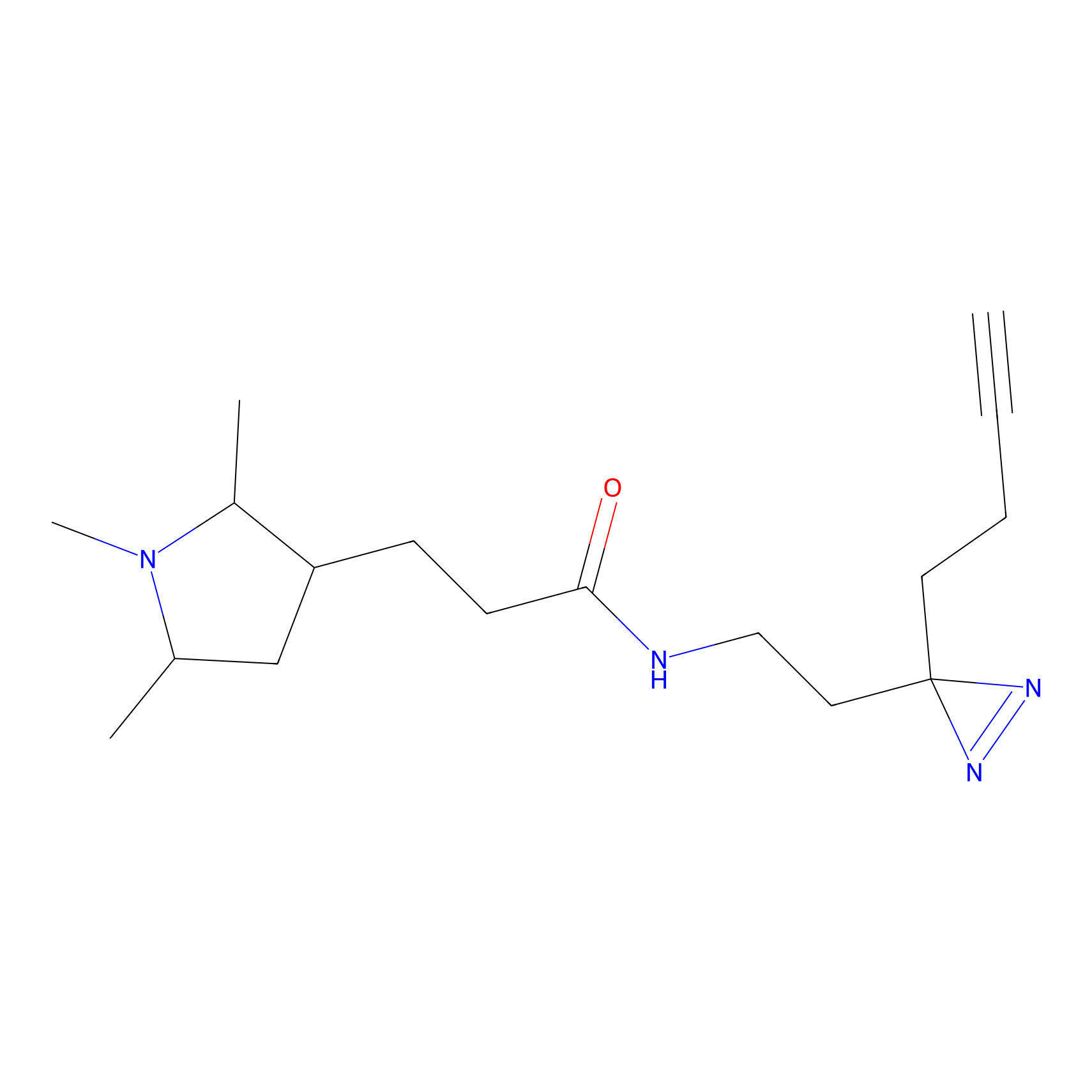
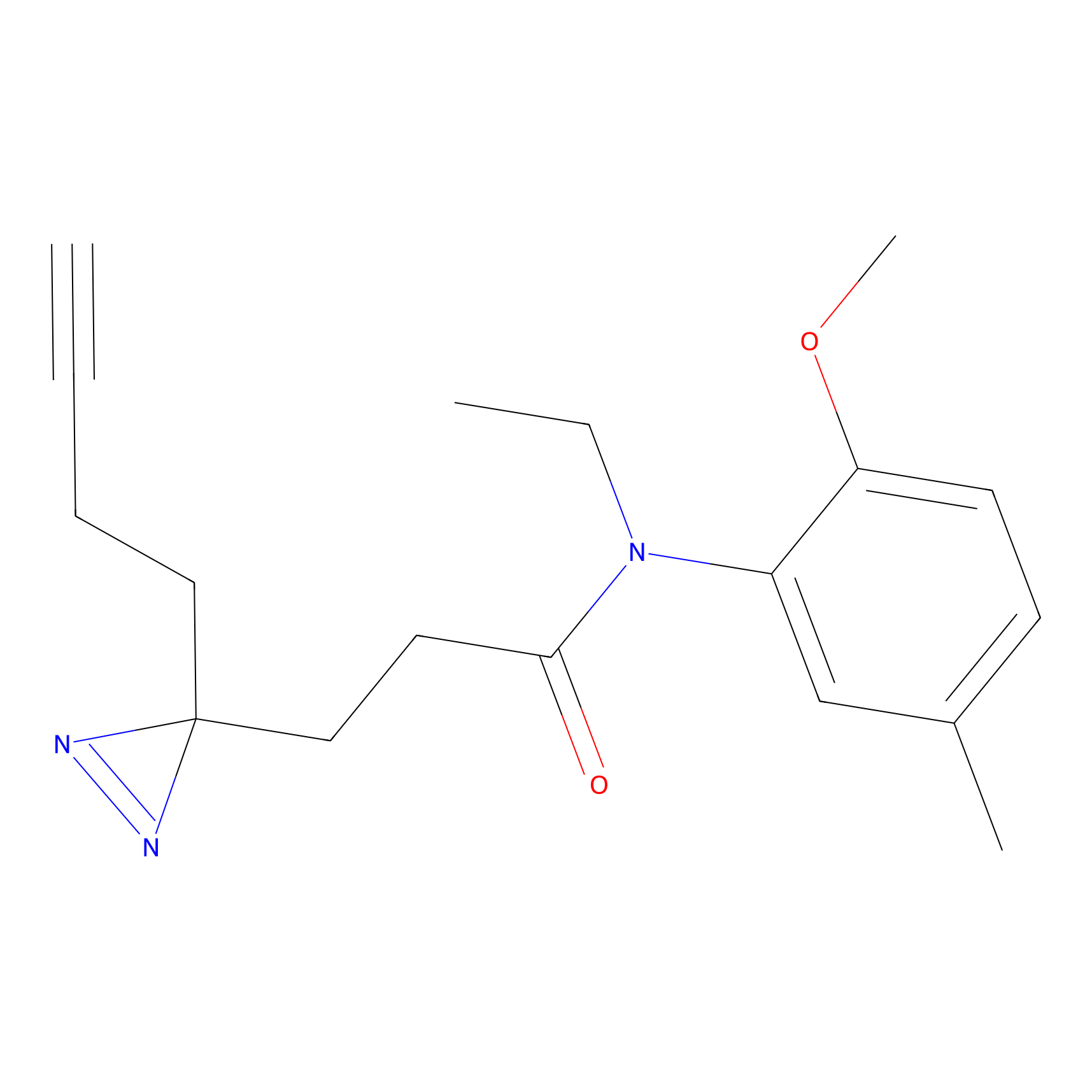
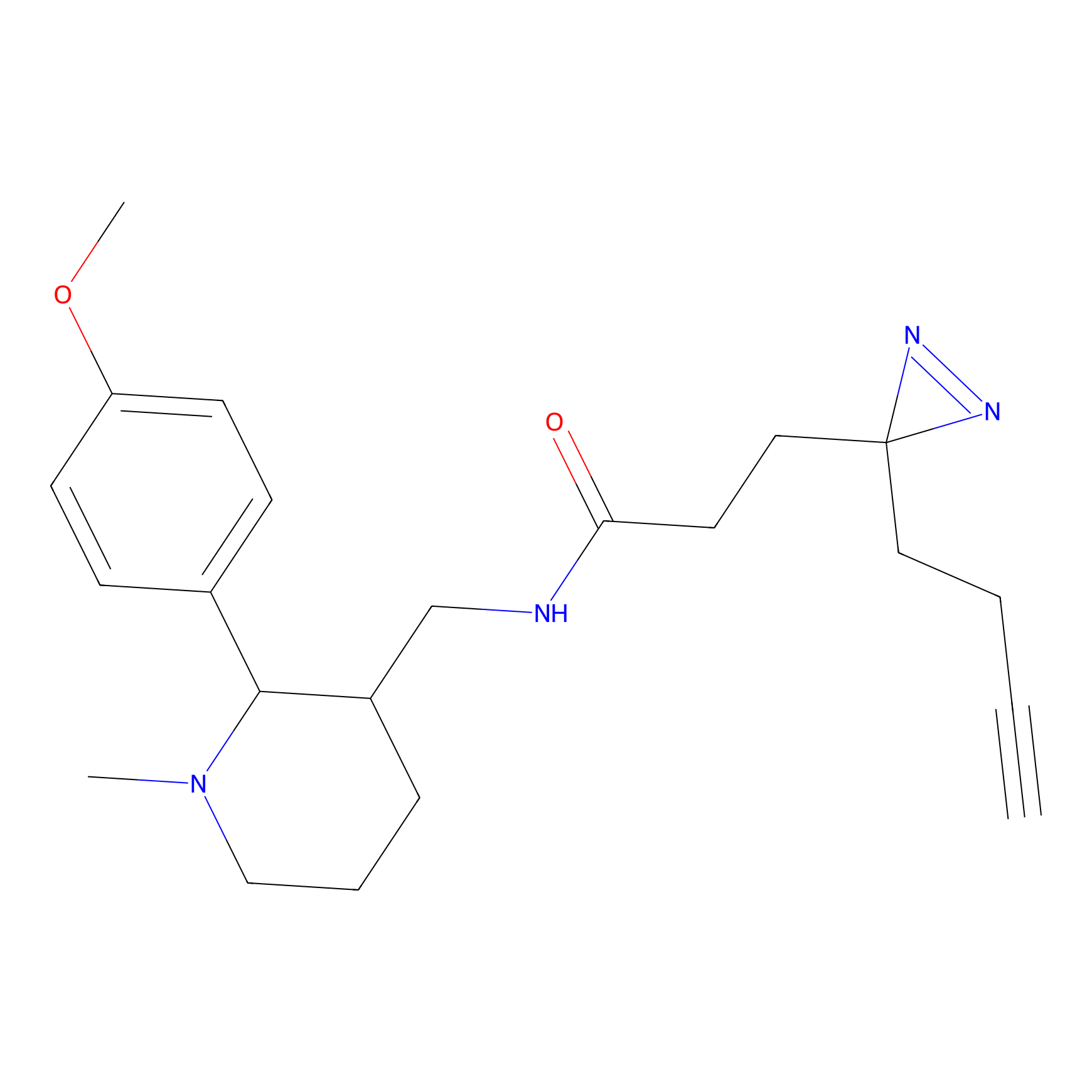
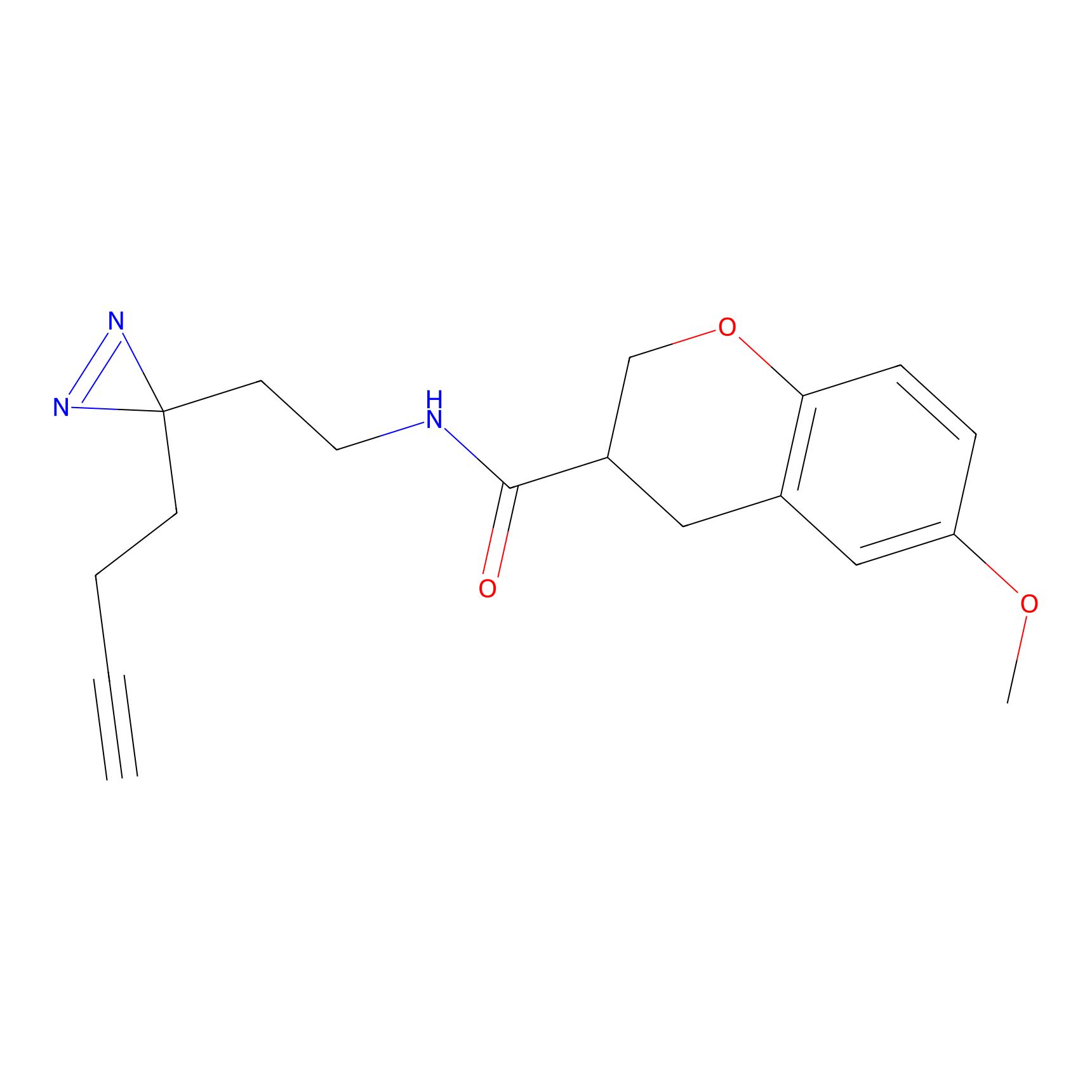
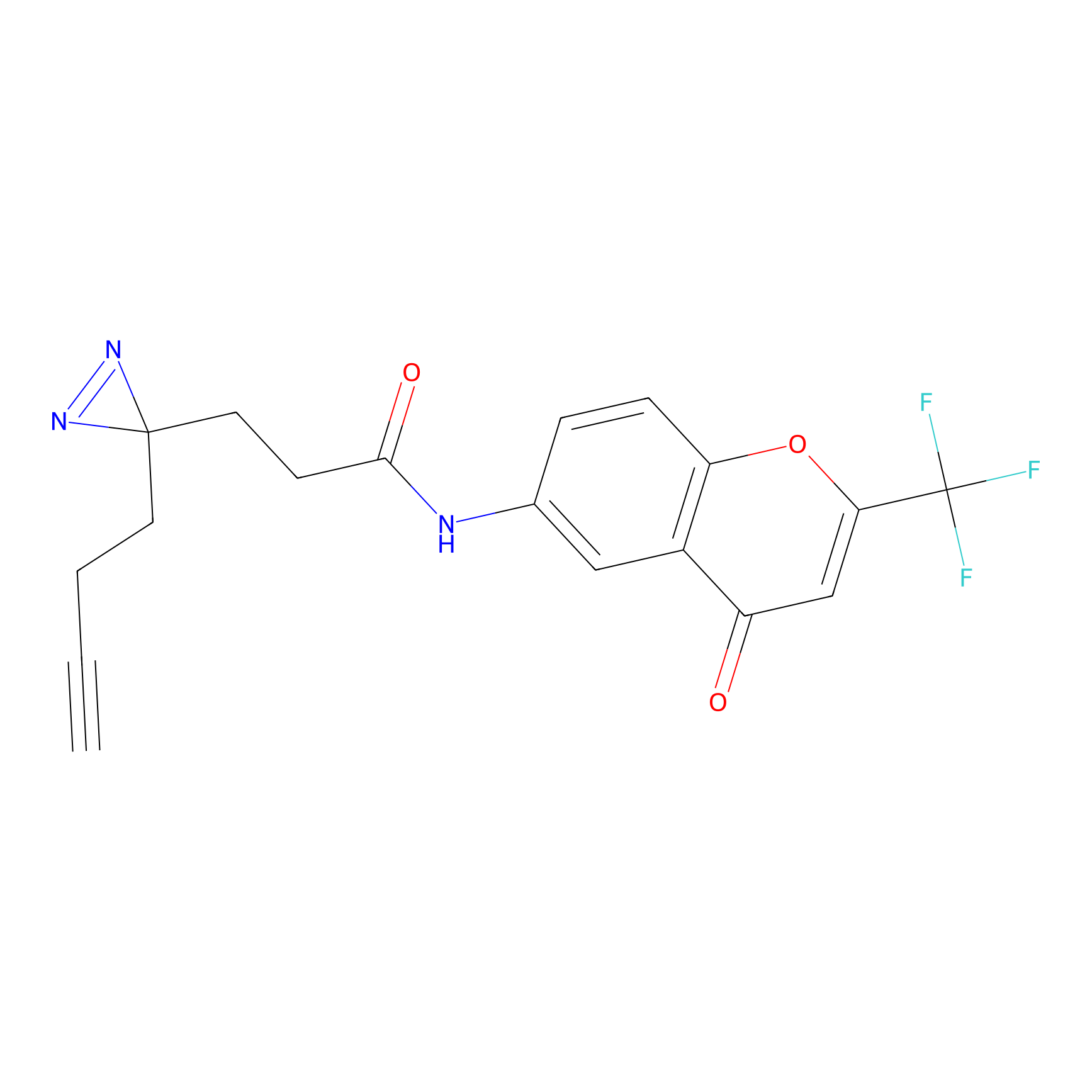
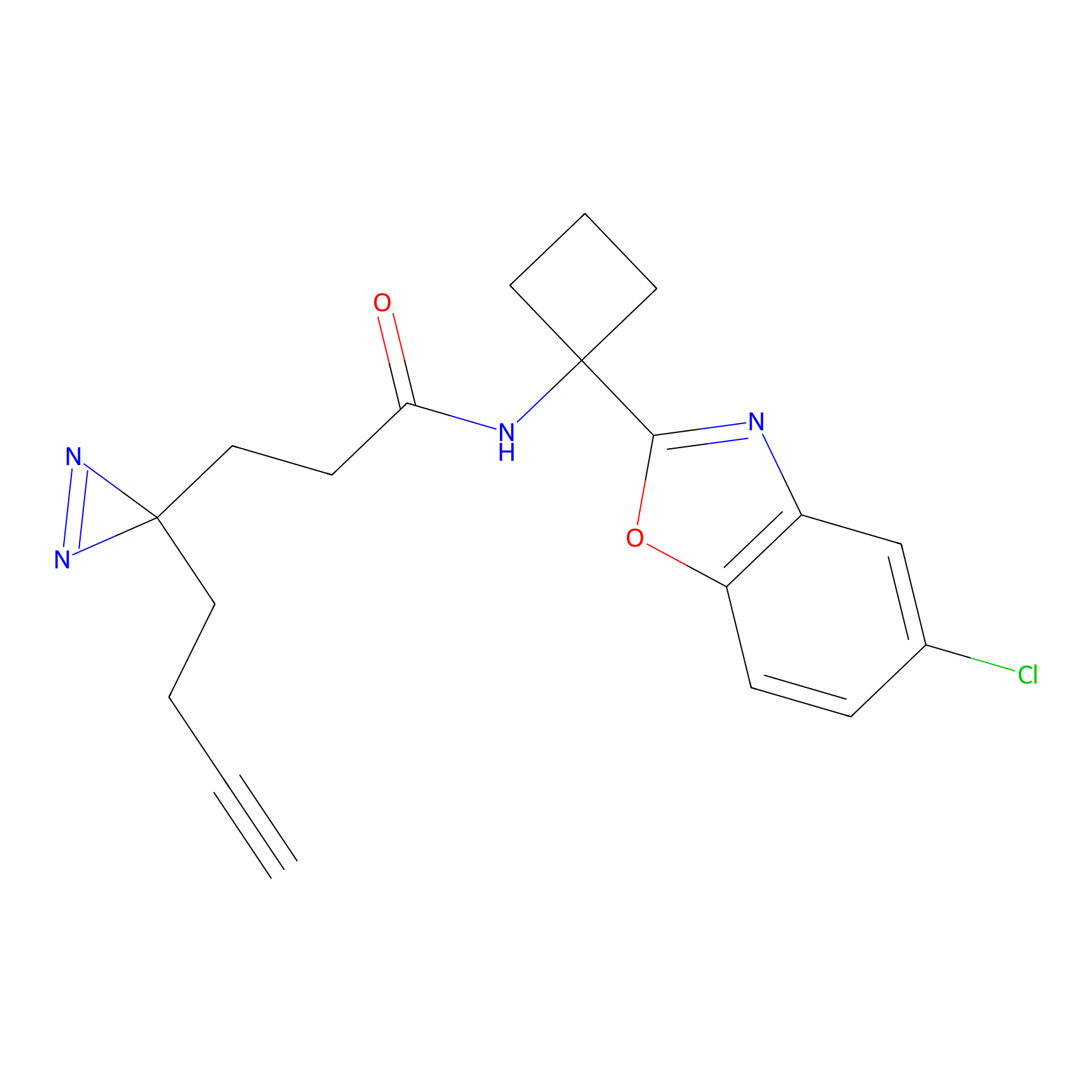
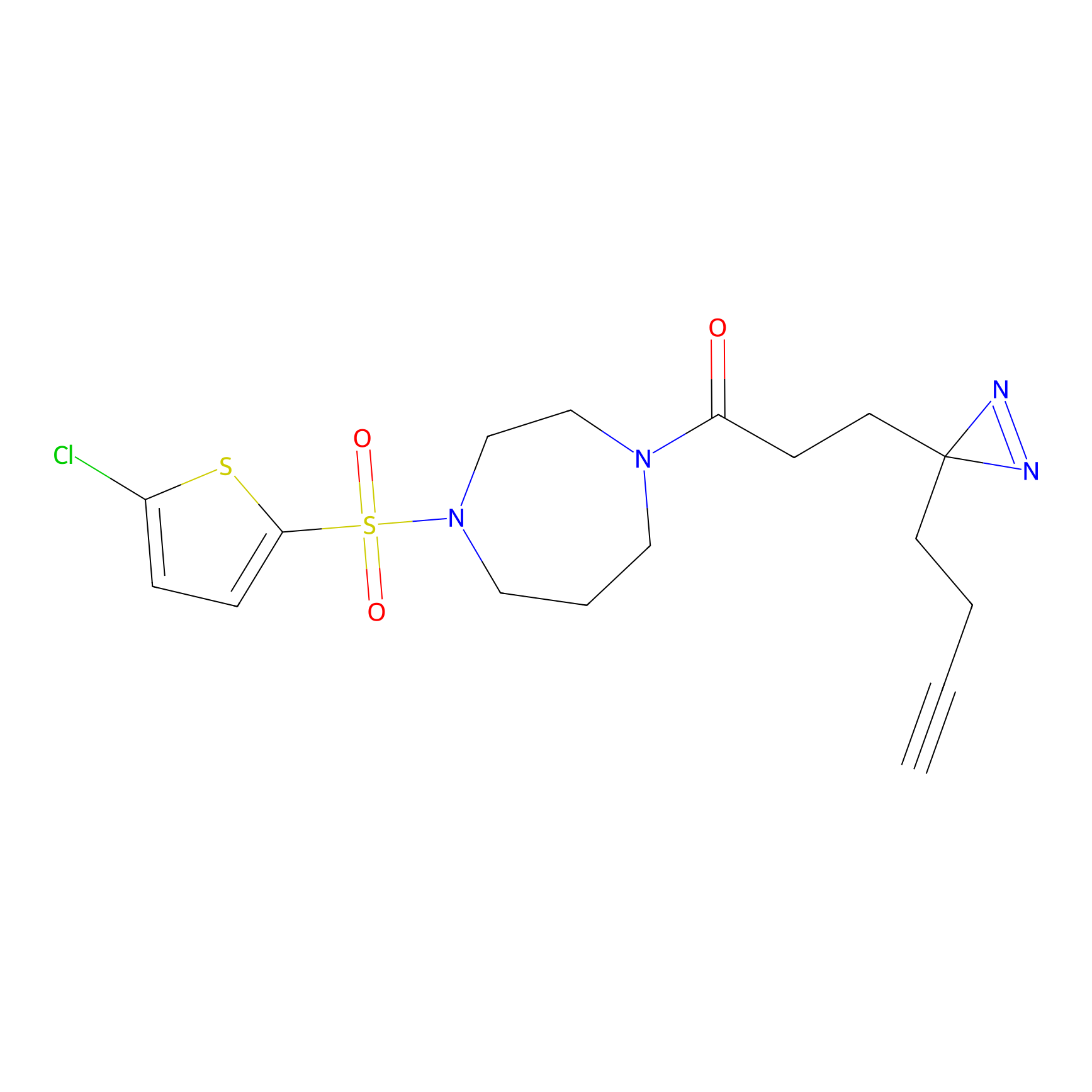
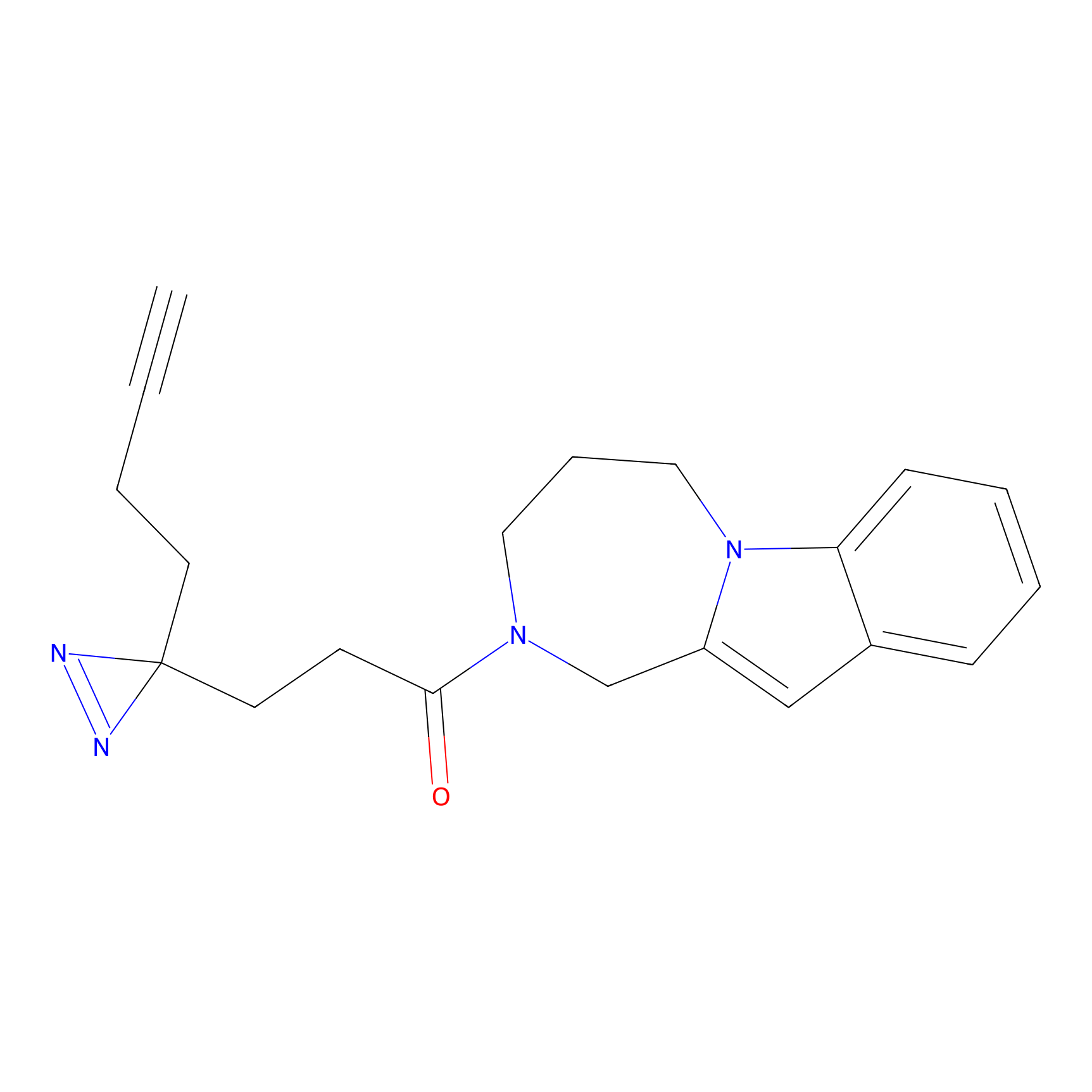
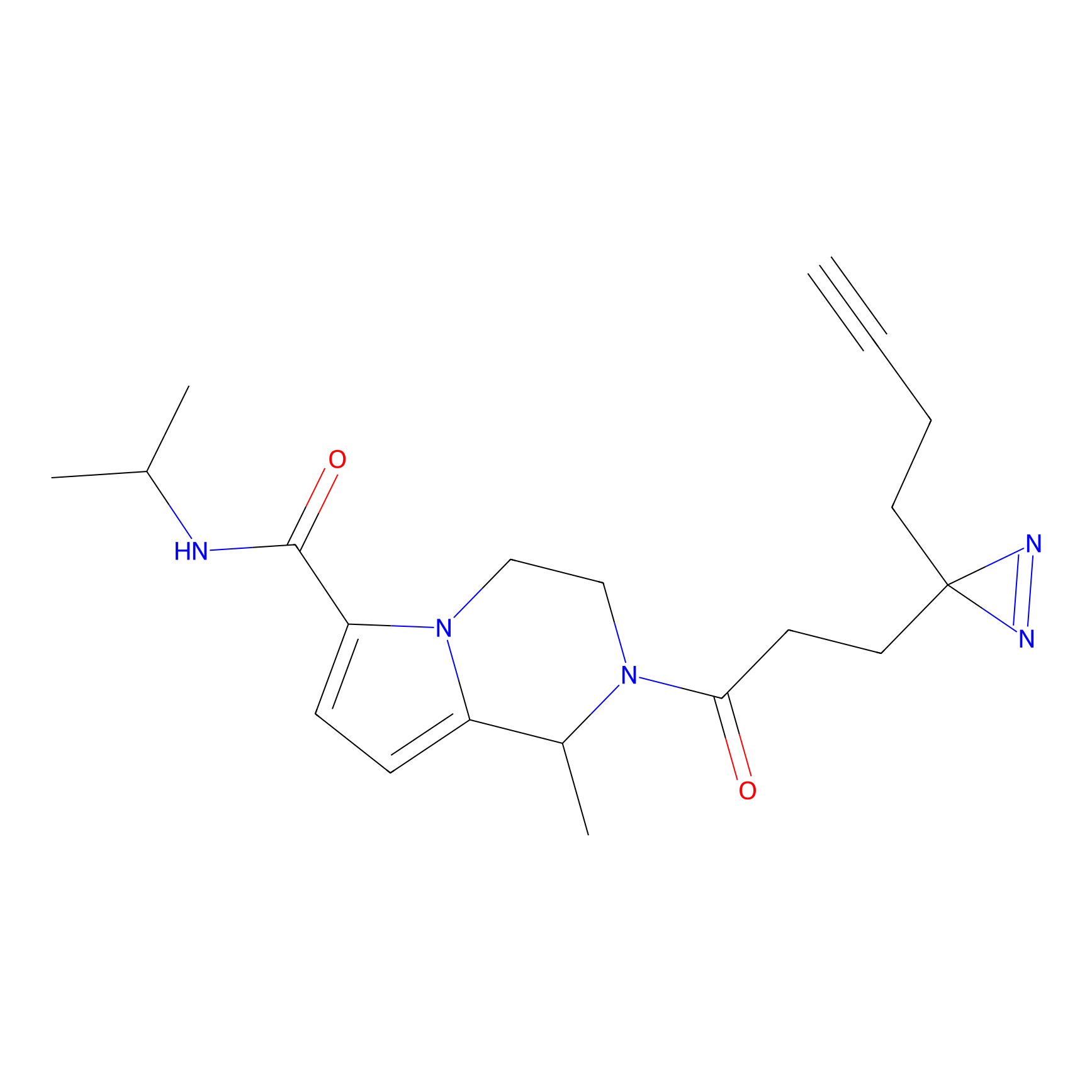
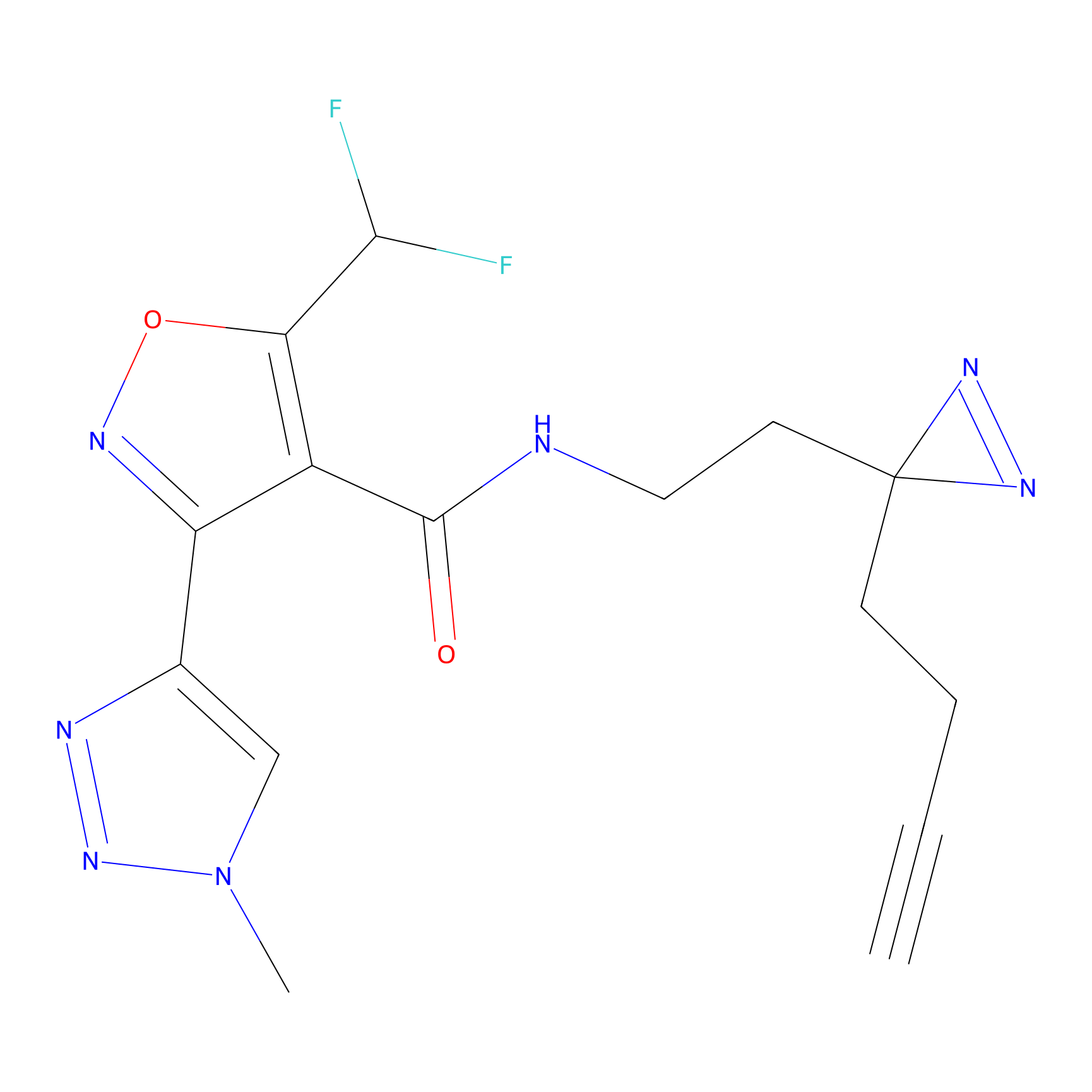
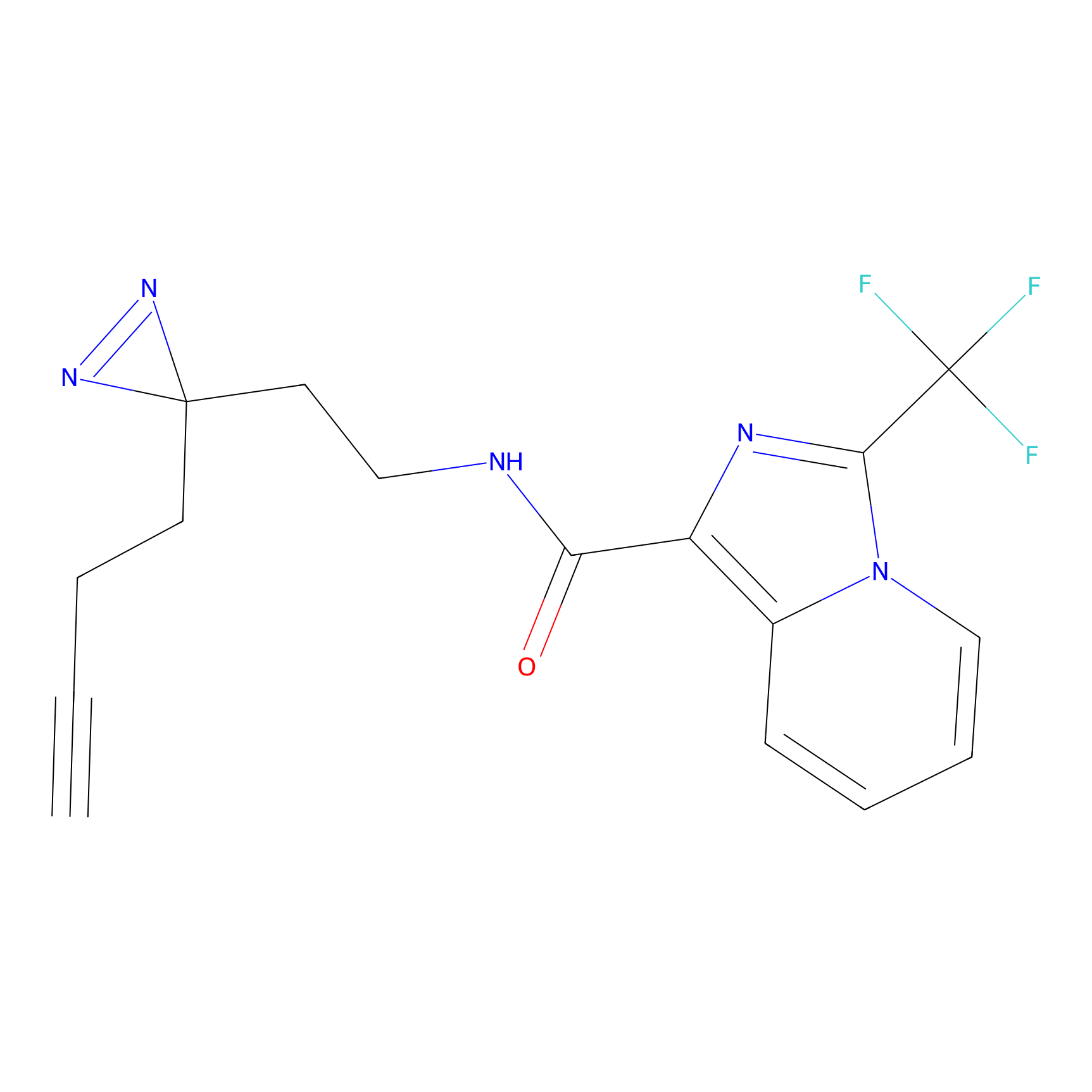
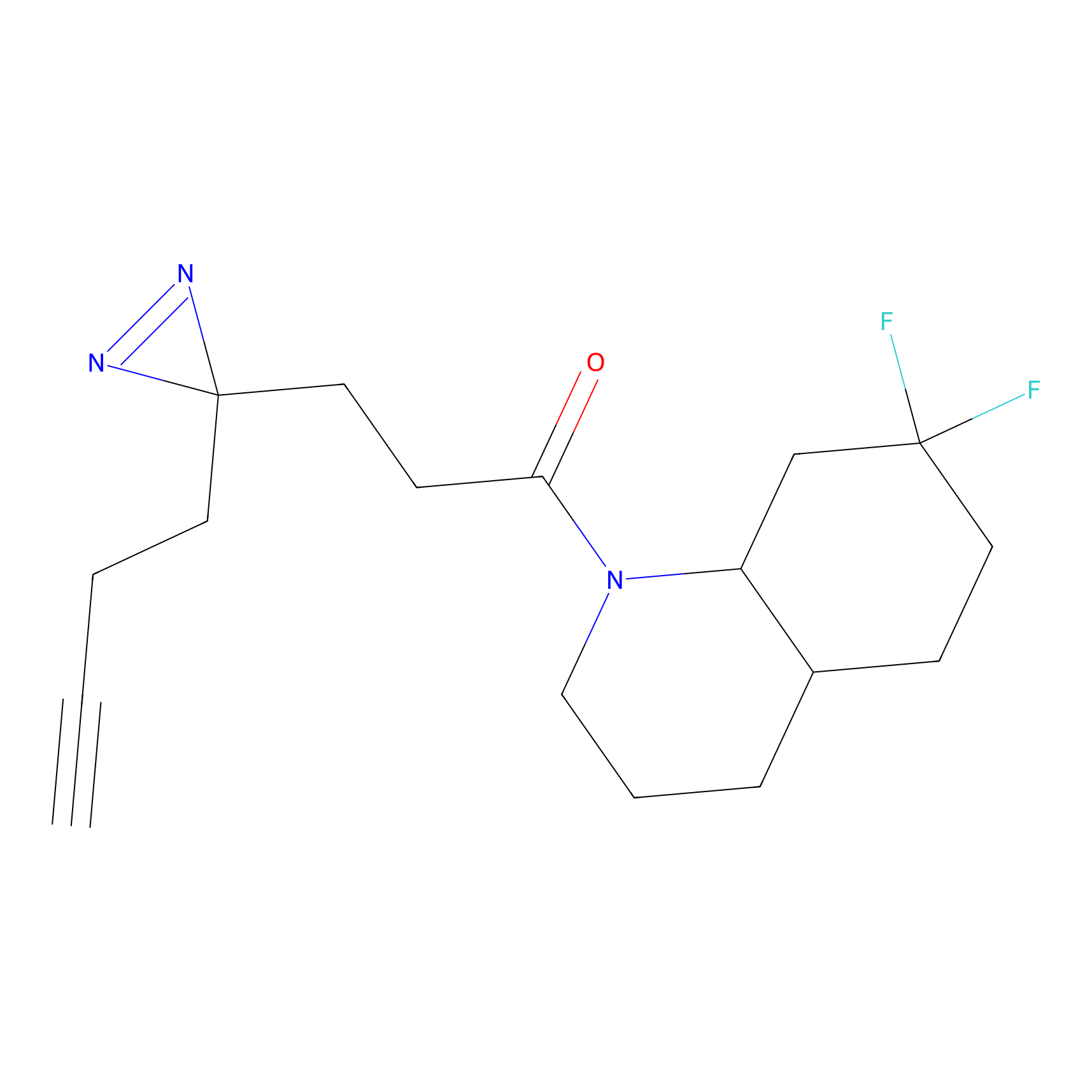
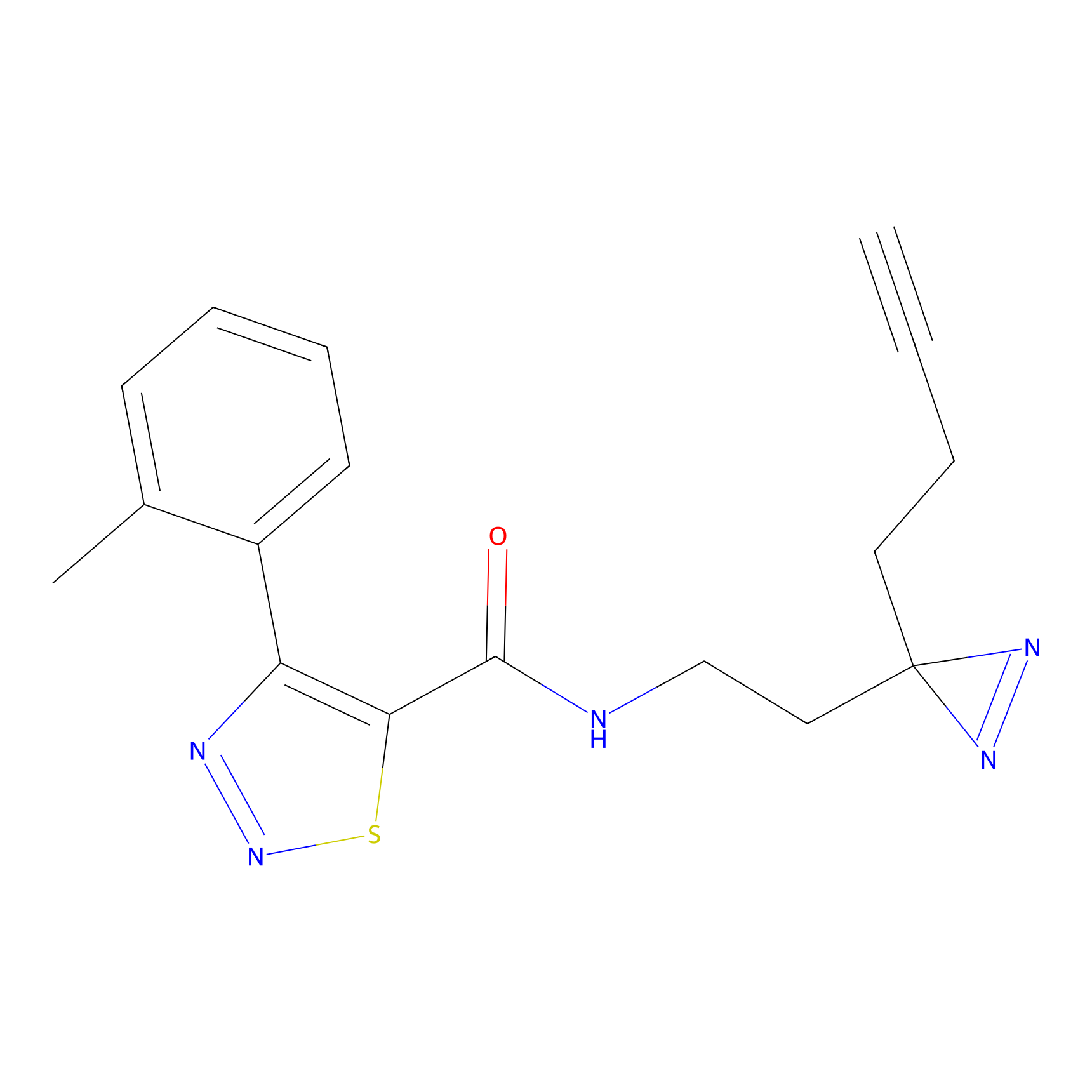
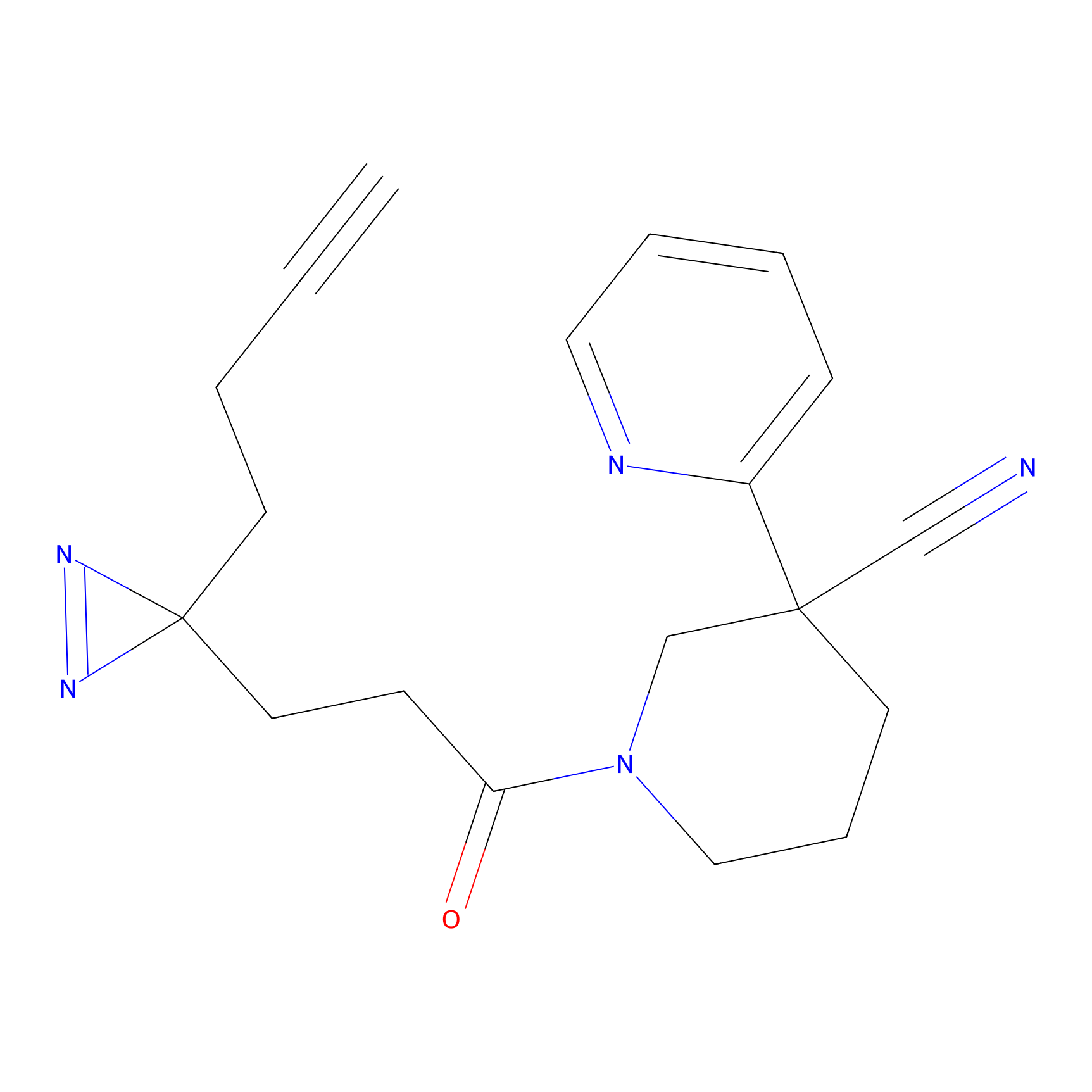
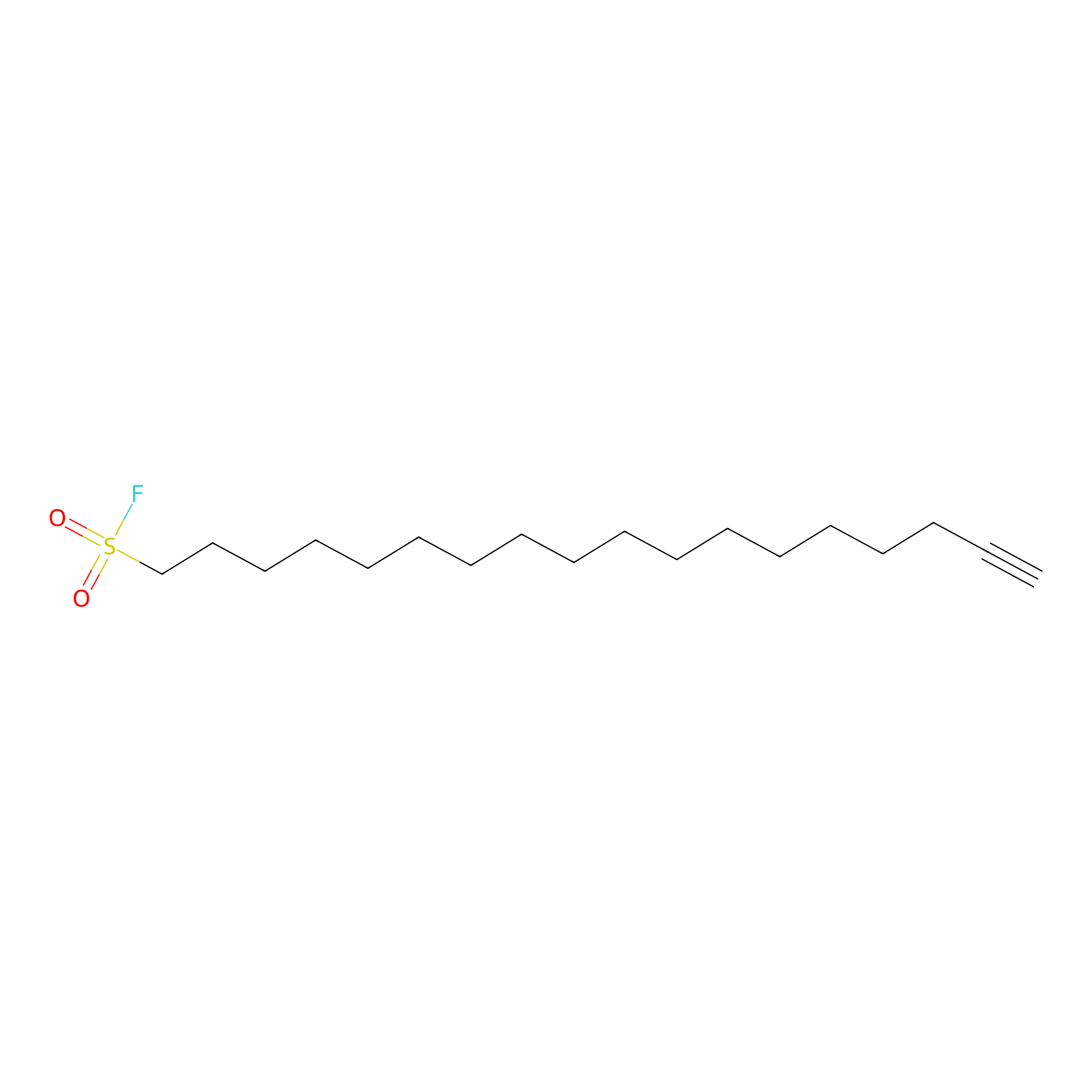
FBPP2 Probe Info |
 |
26.02 | LDD0318 | [2] | |
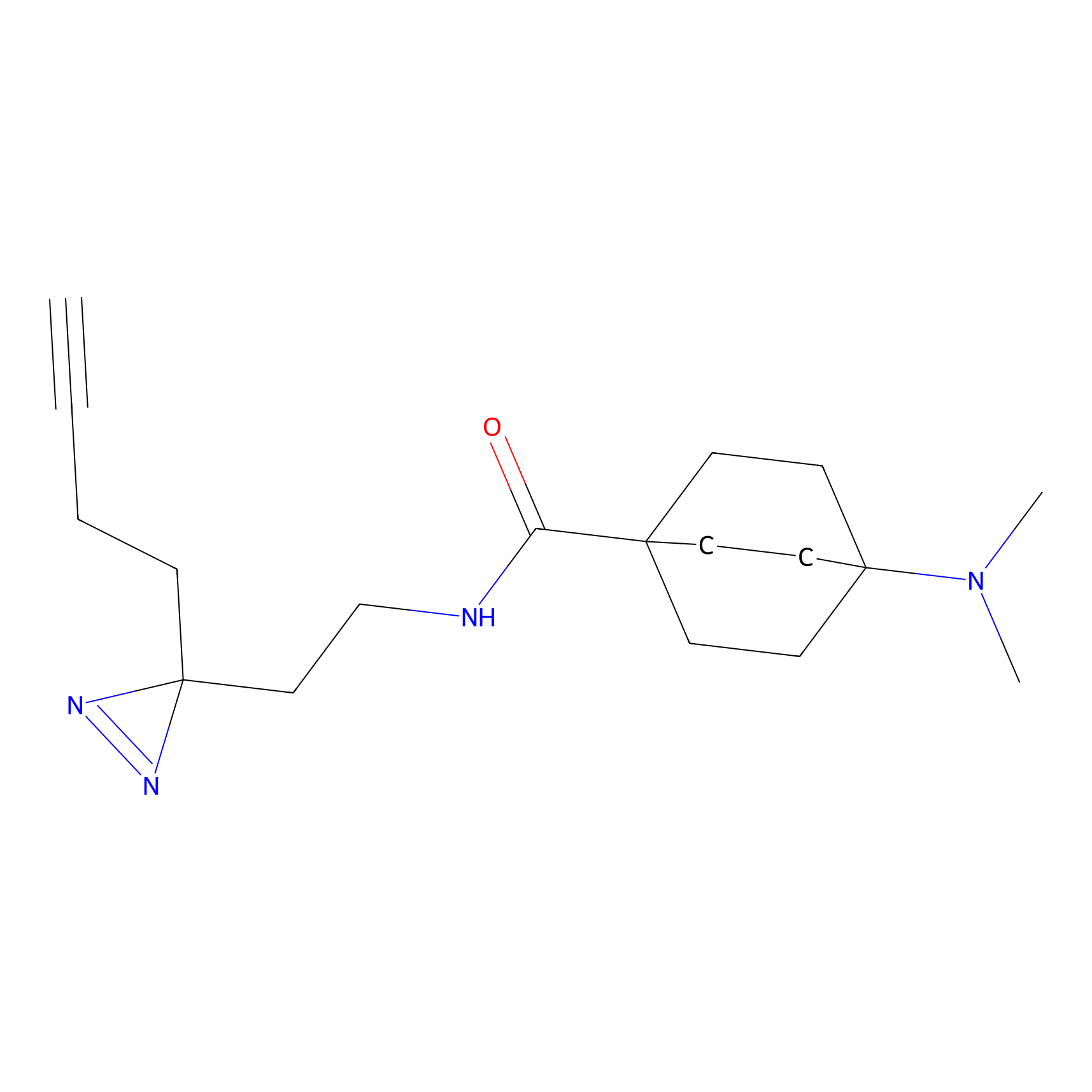
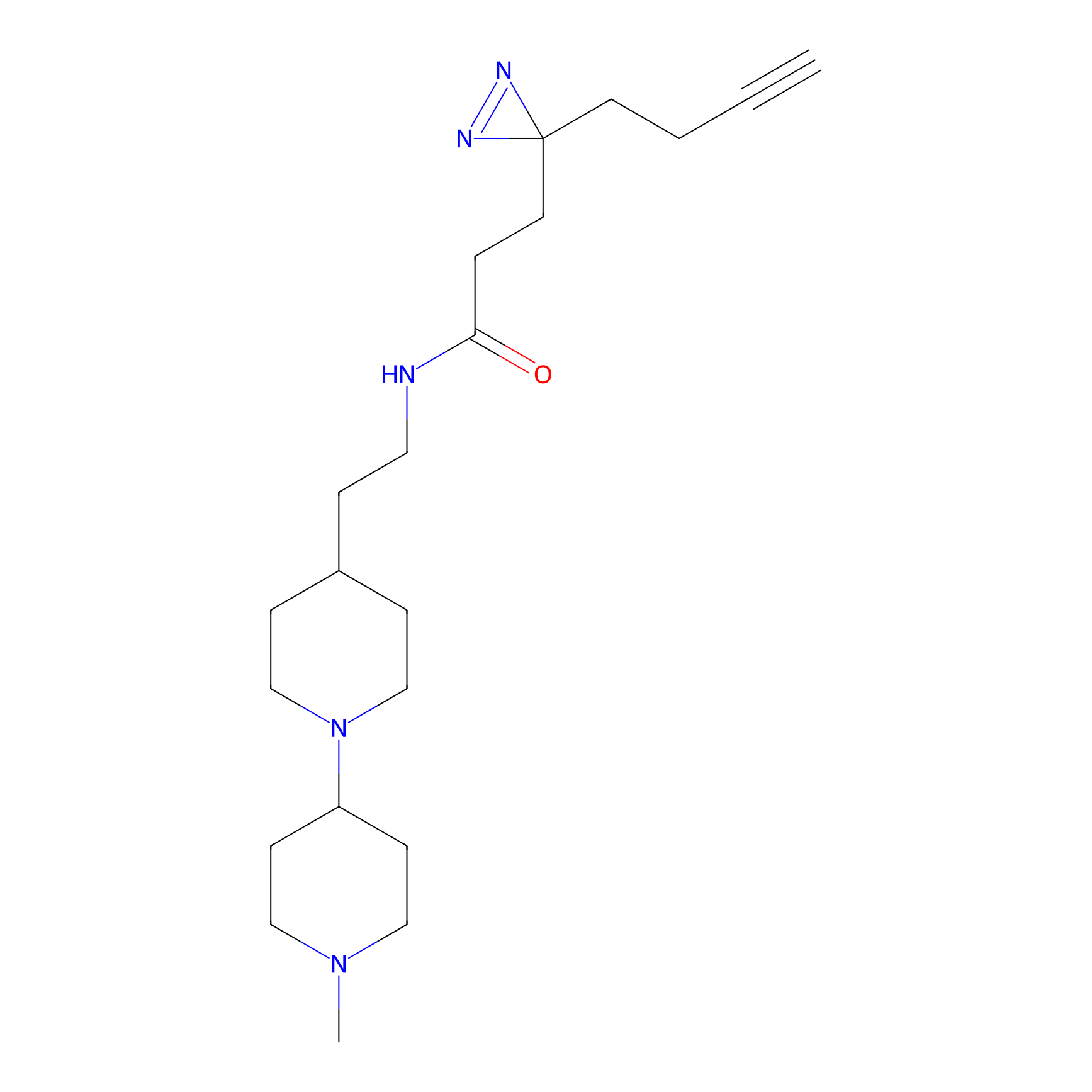
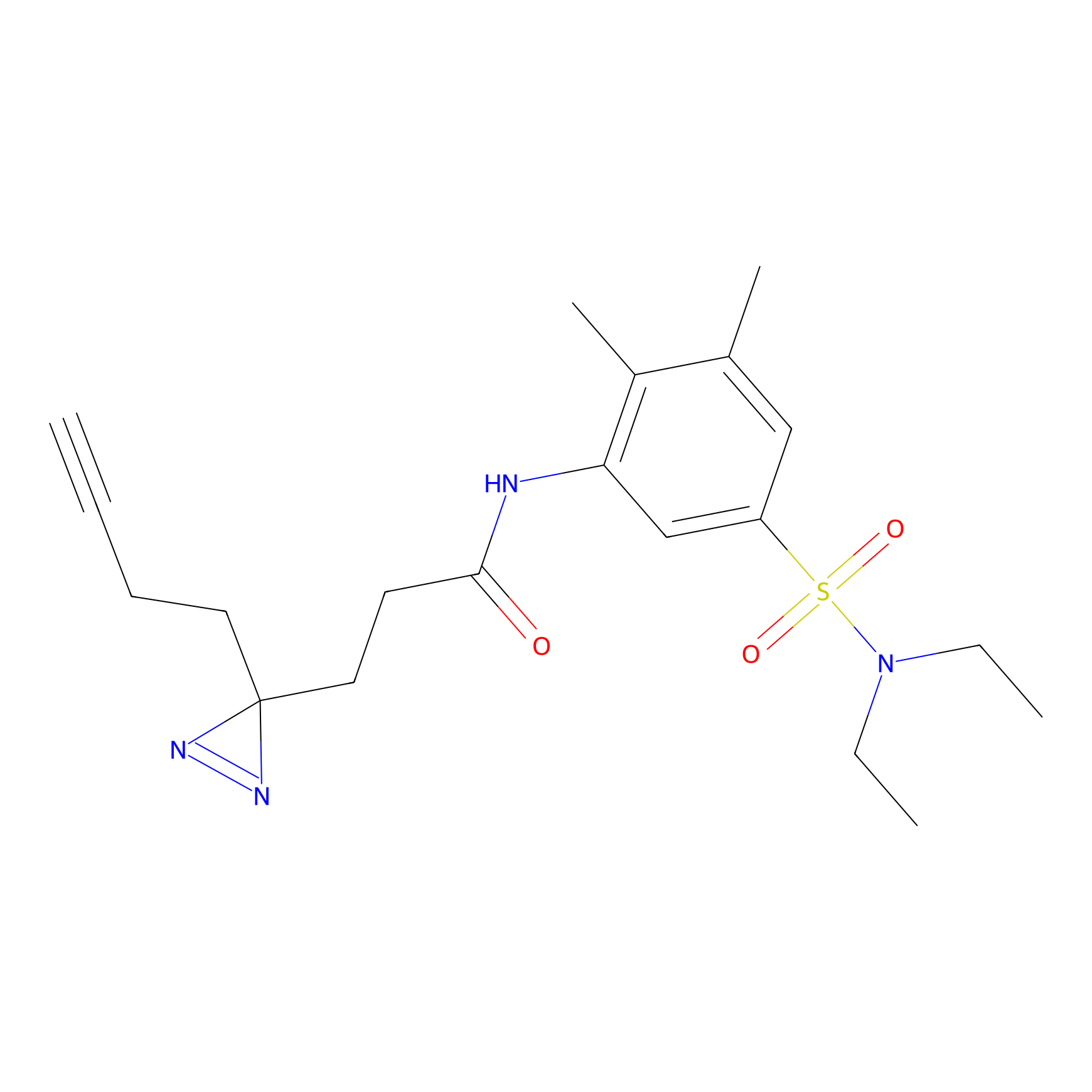
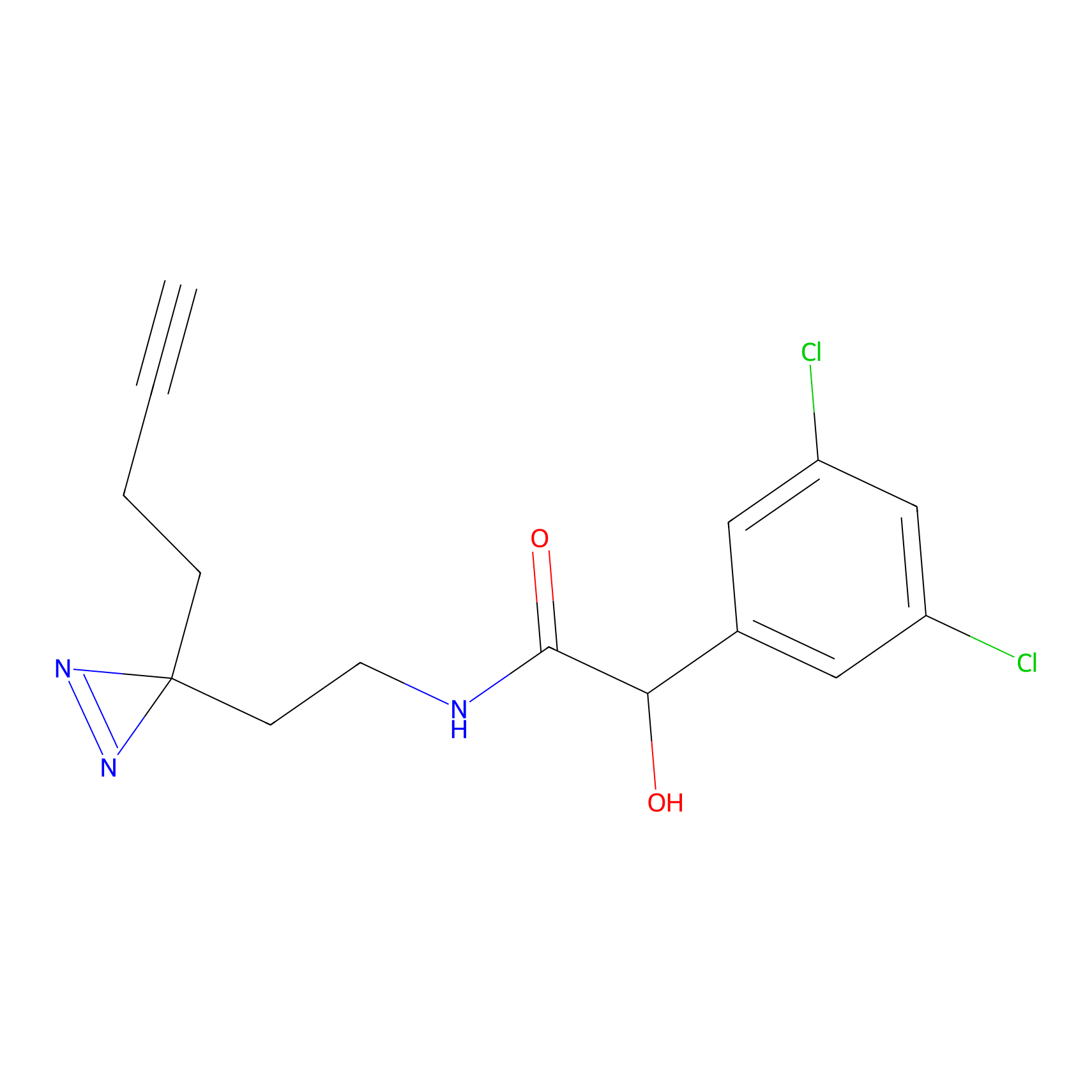
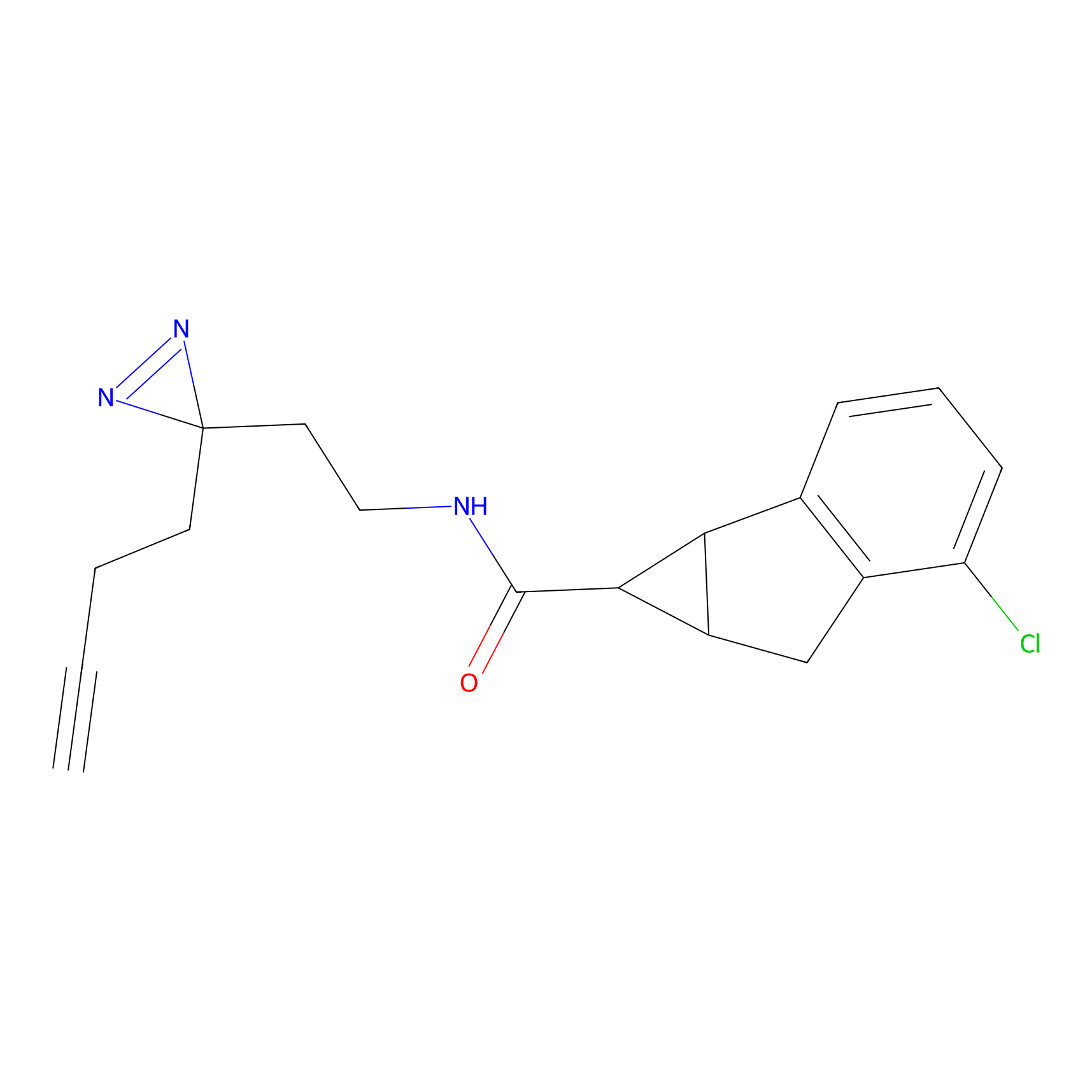
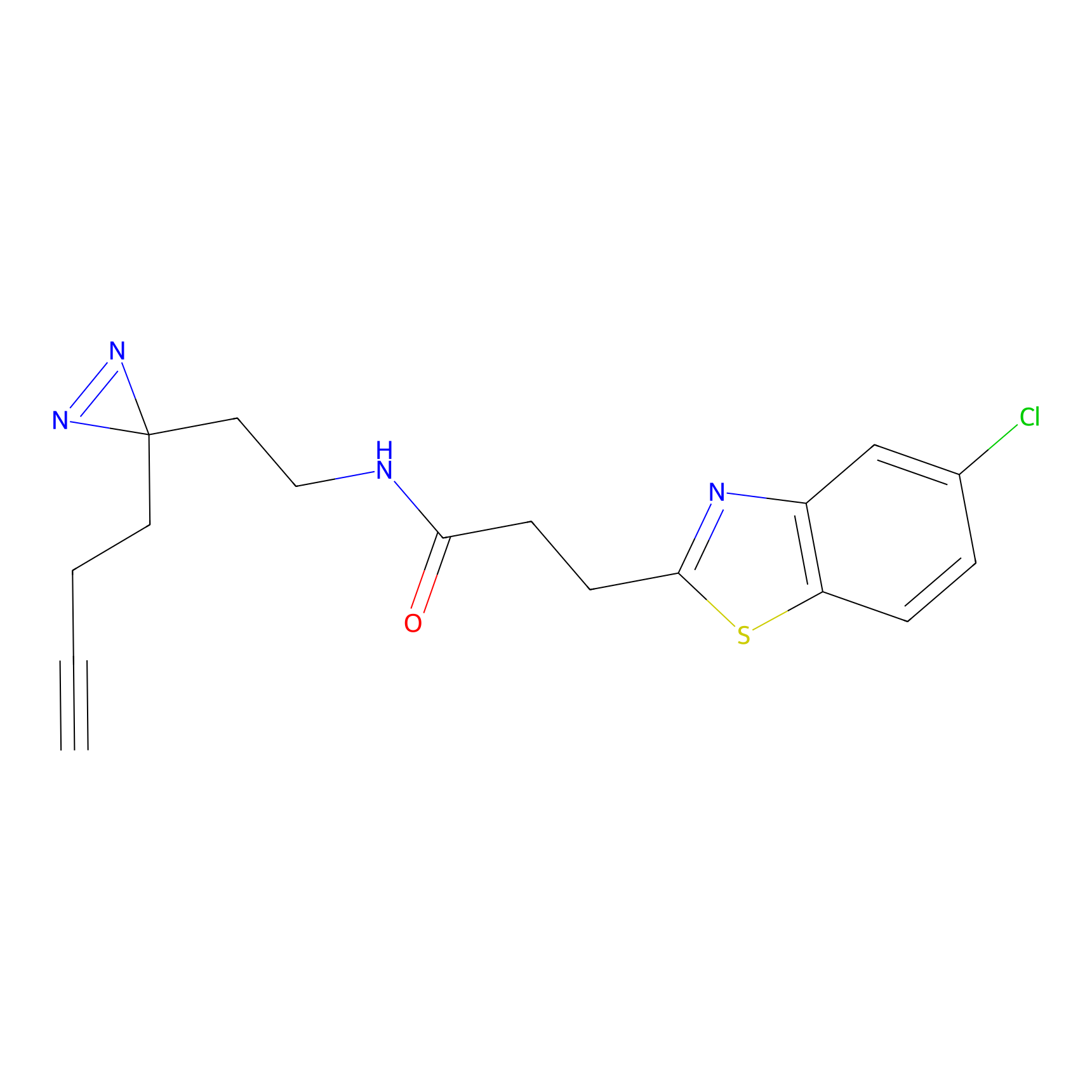
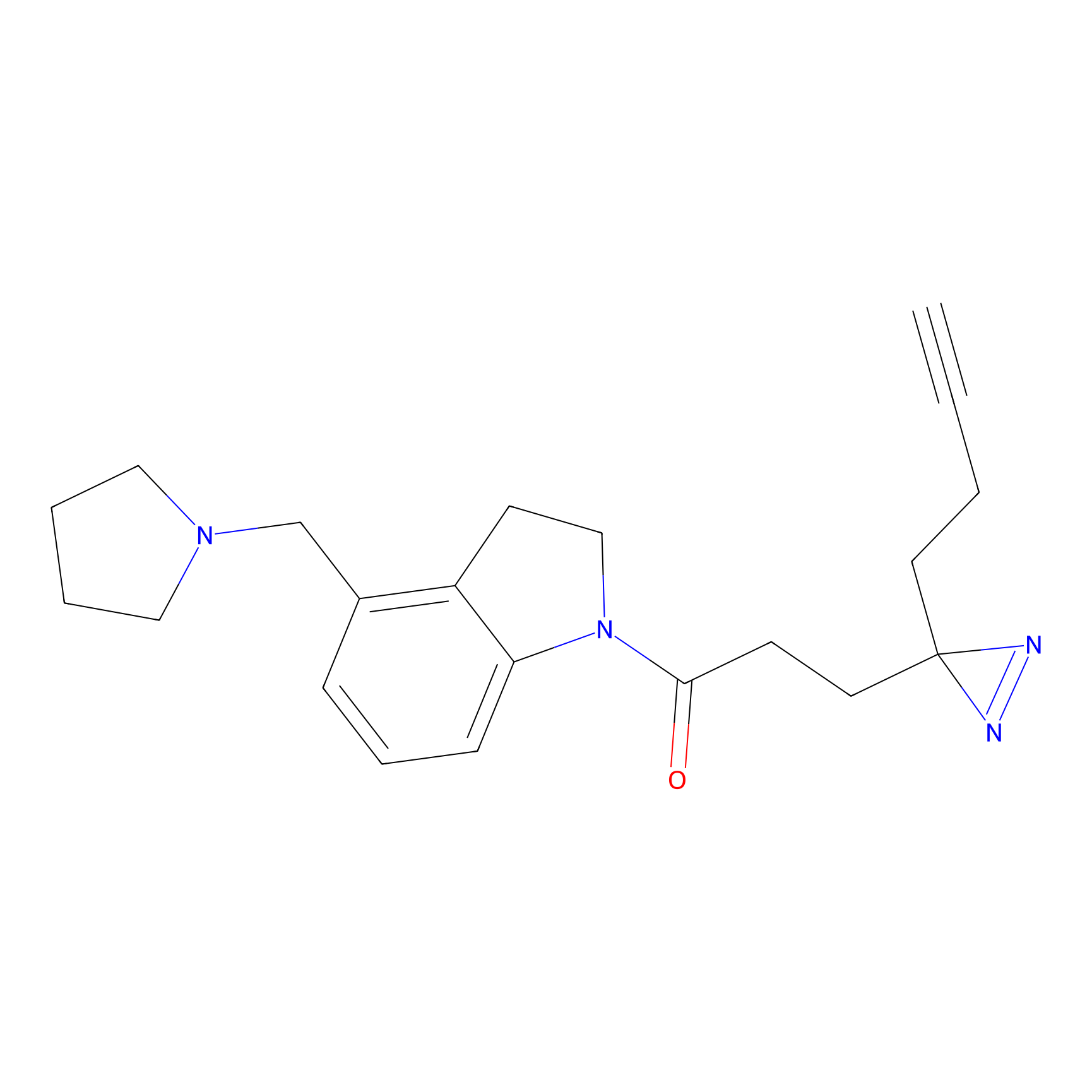
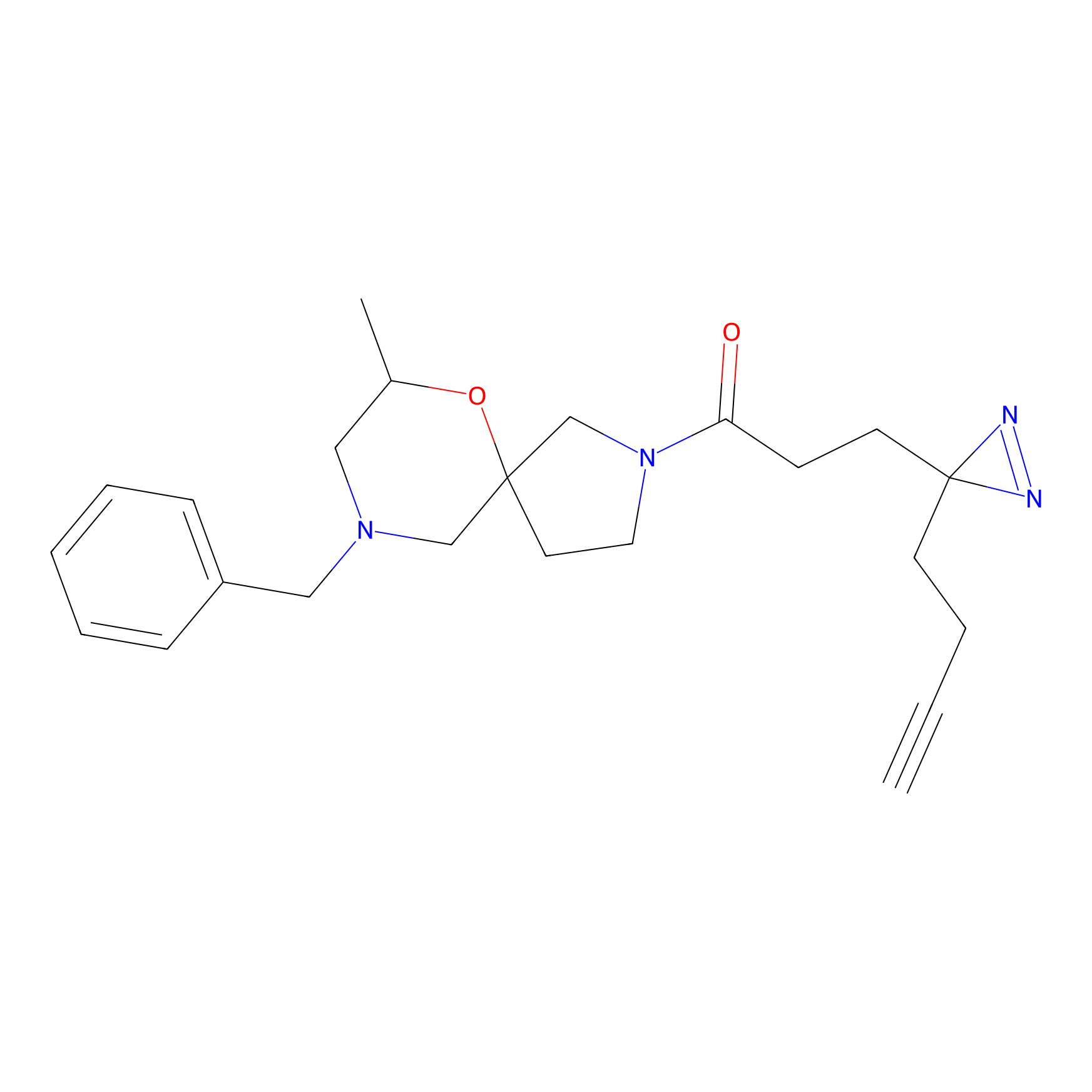
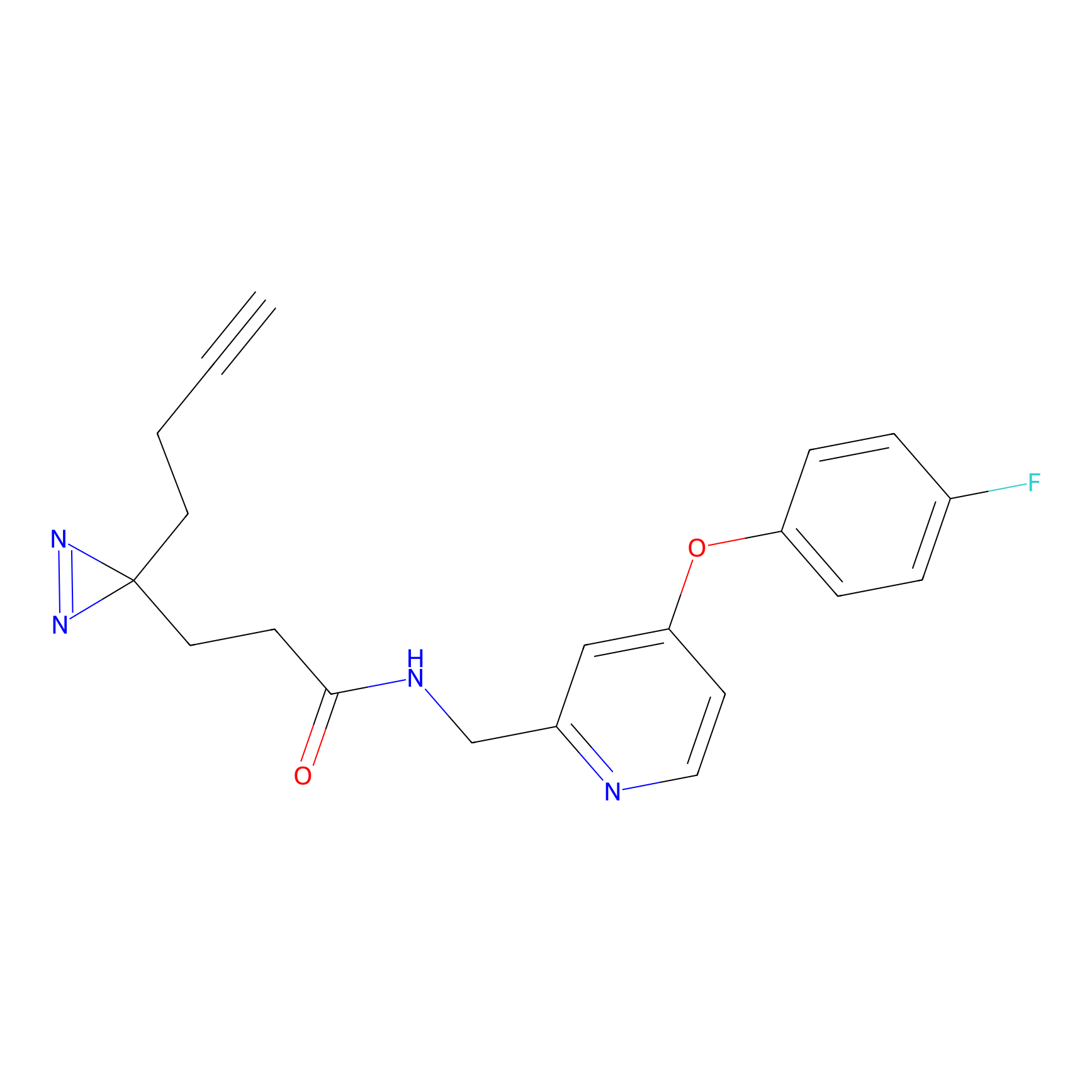
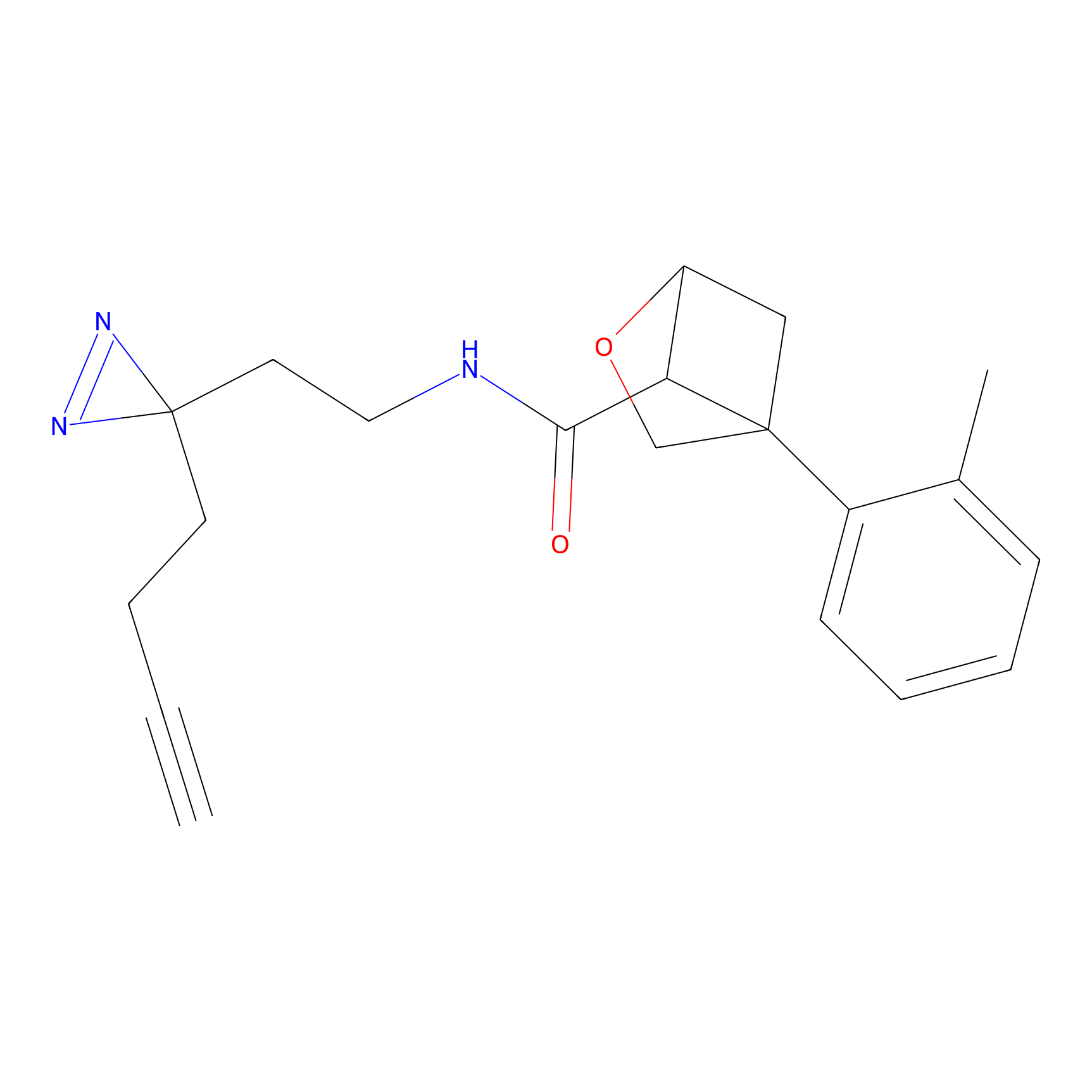
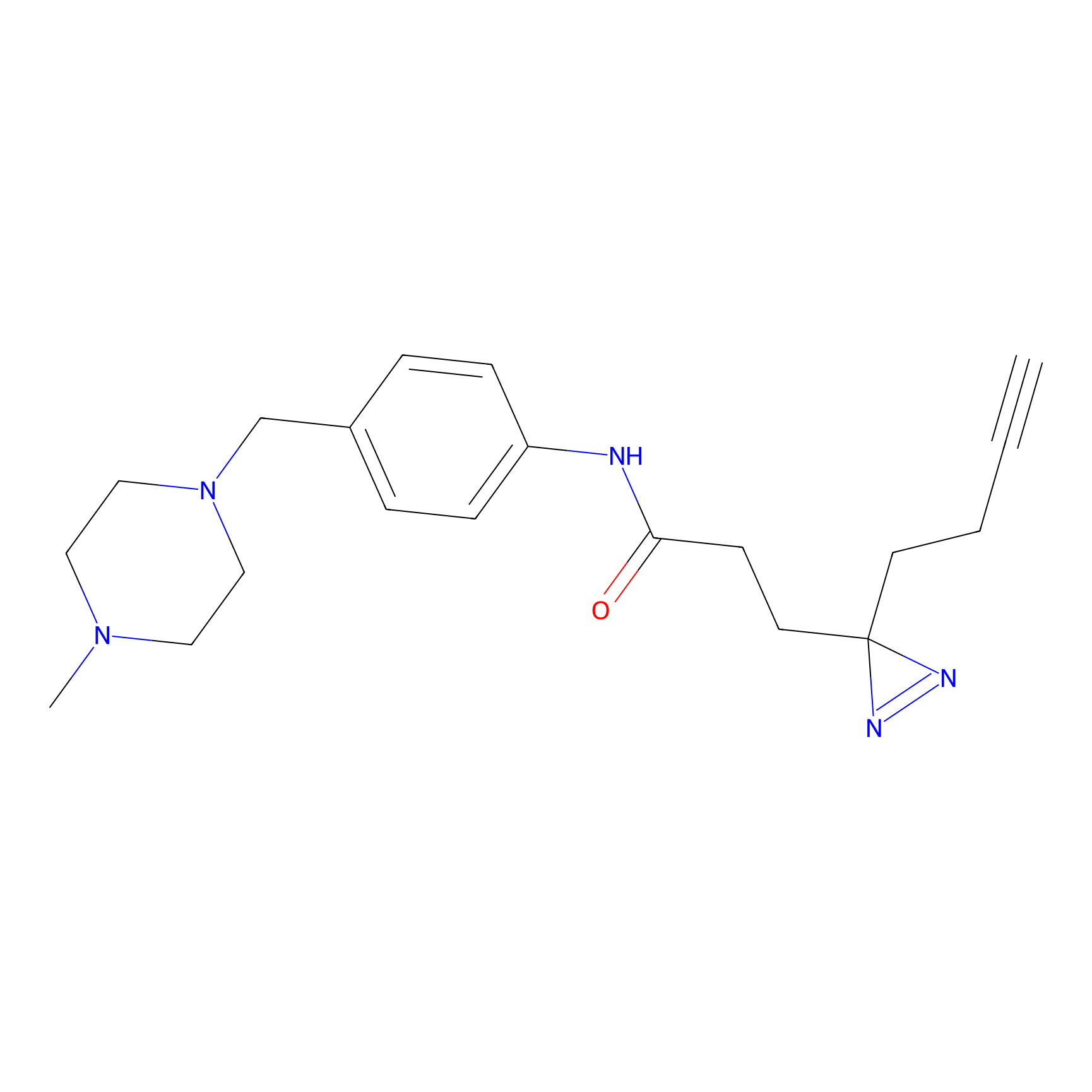
|
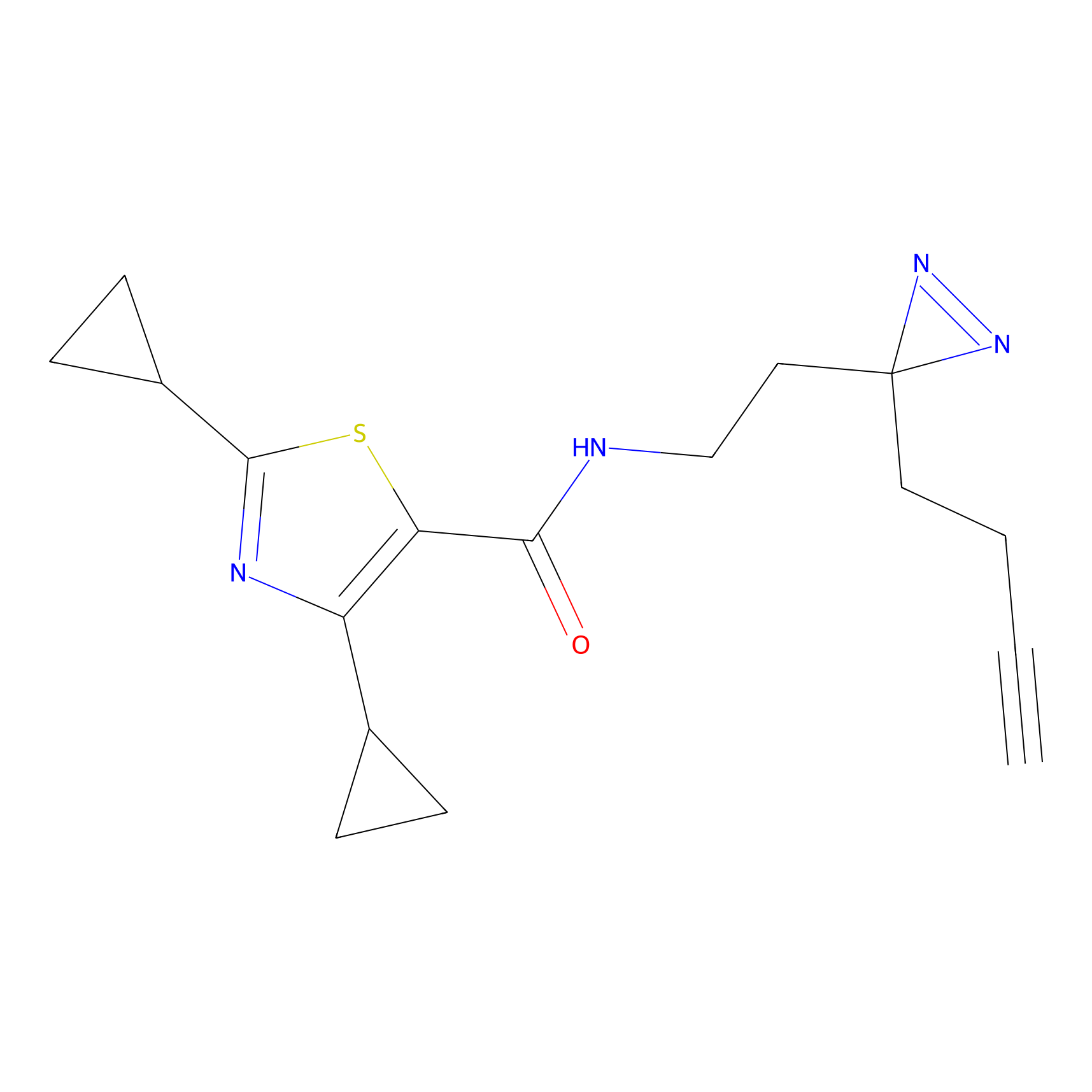
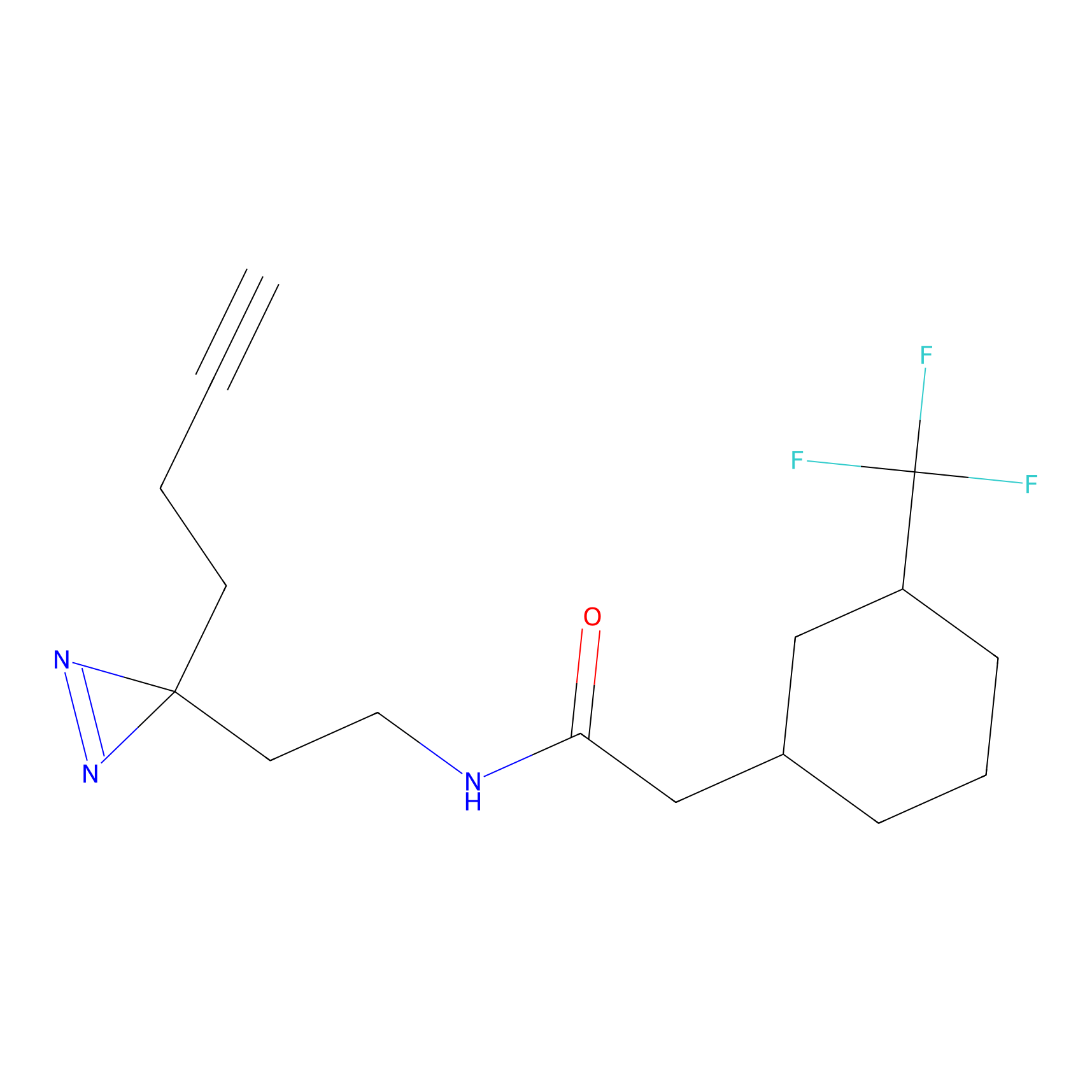
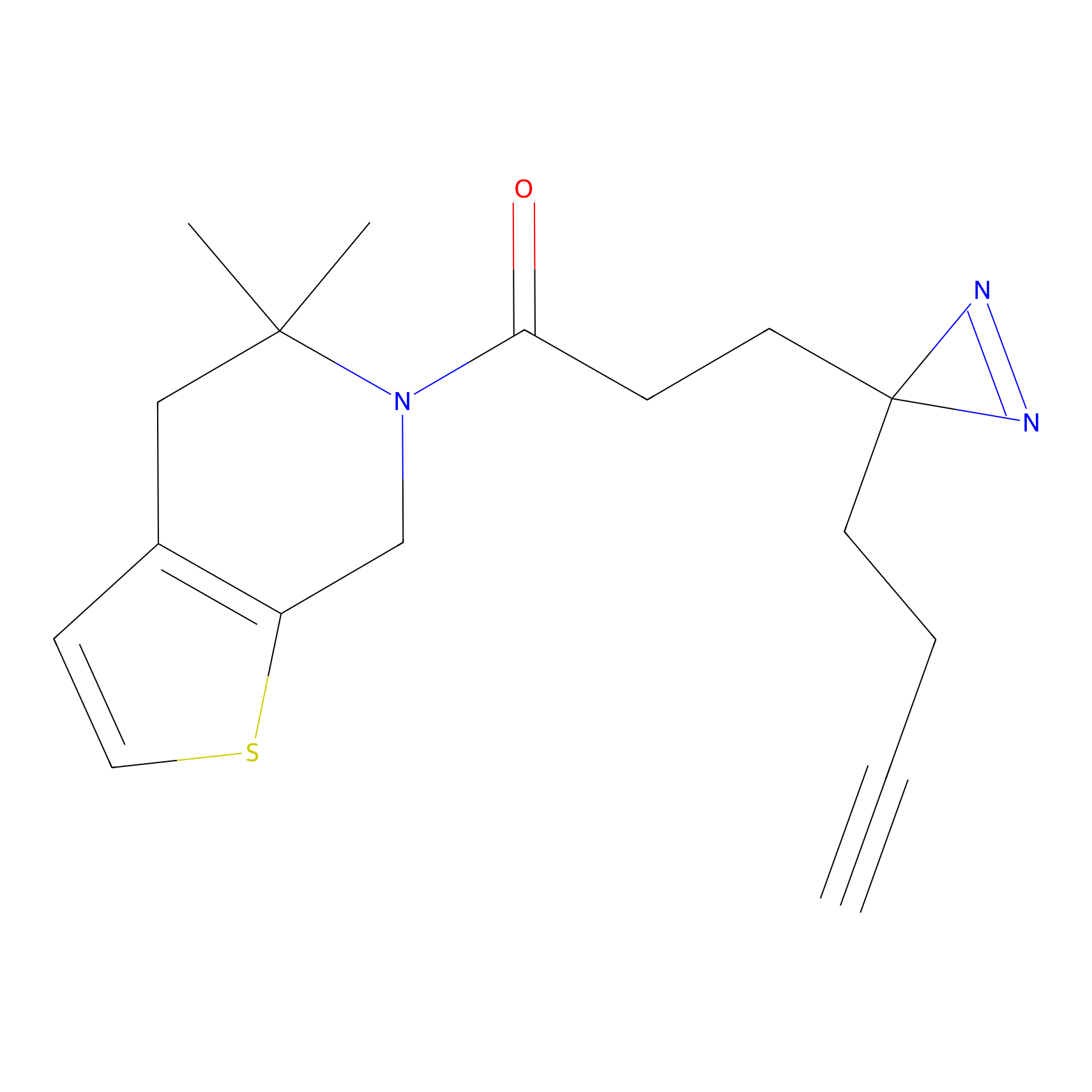
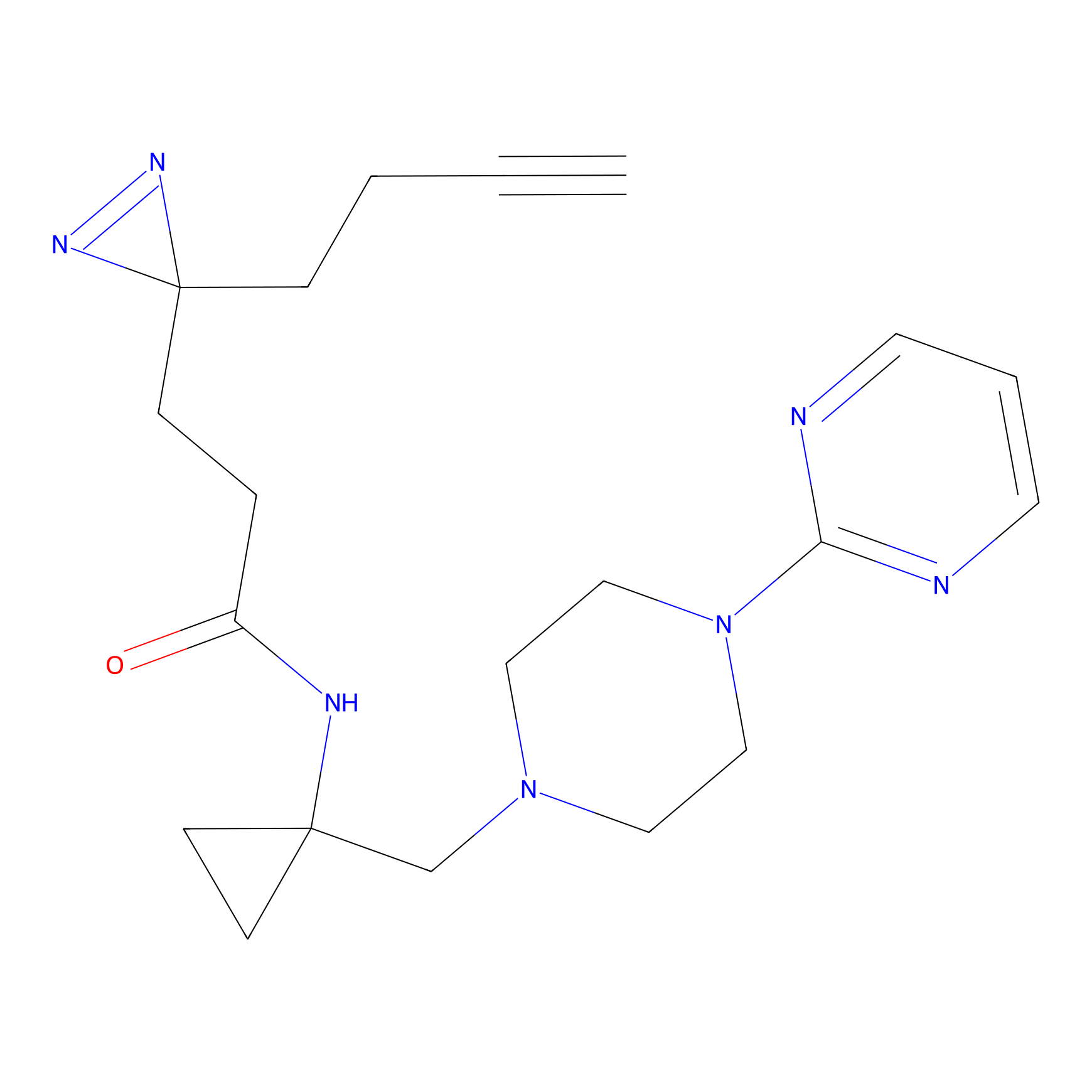
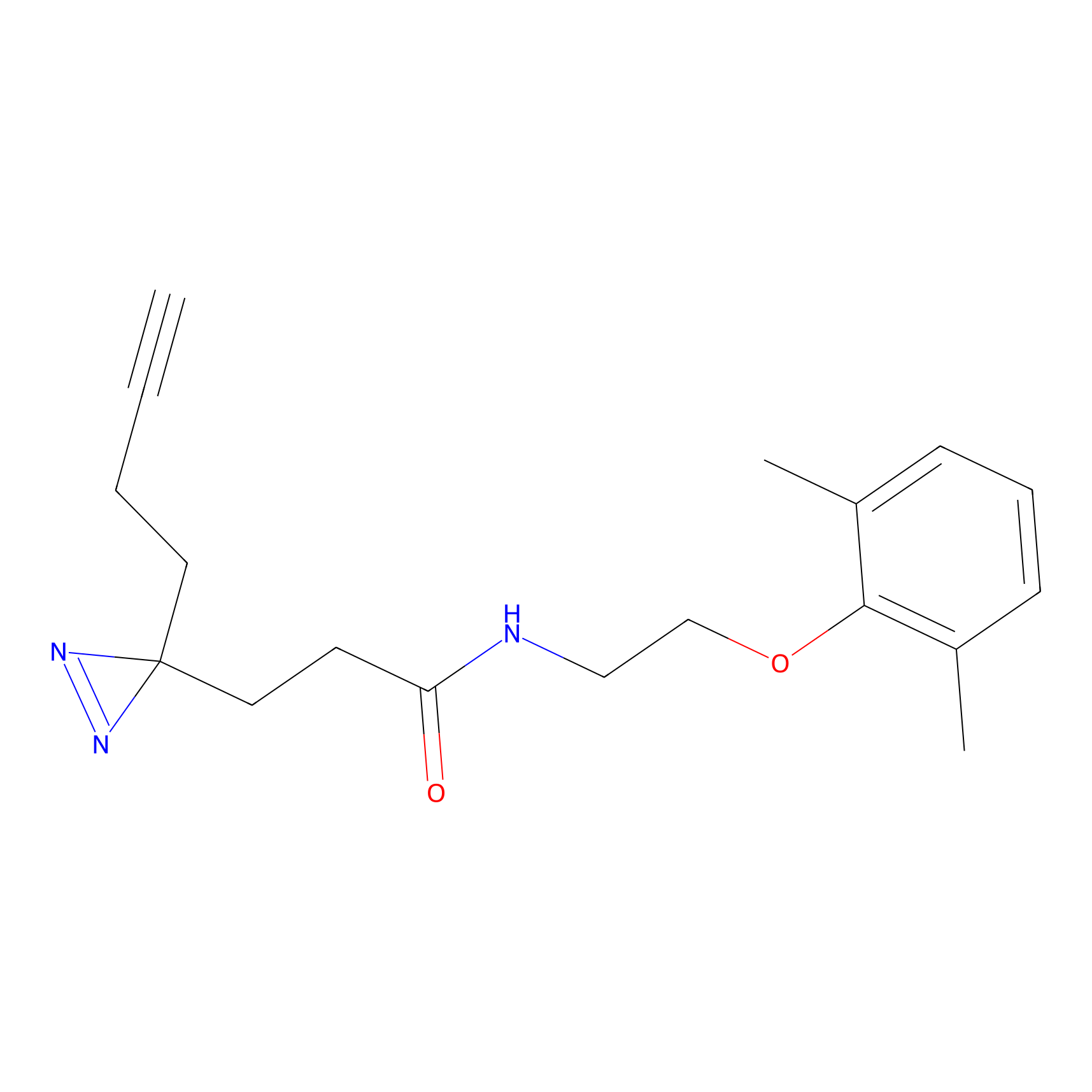
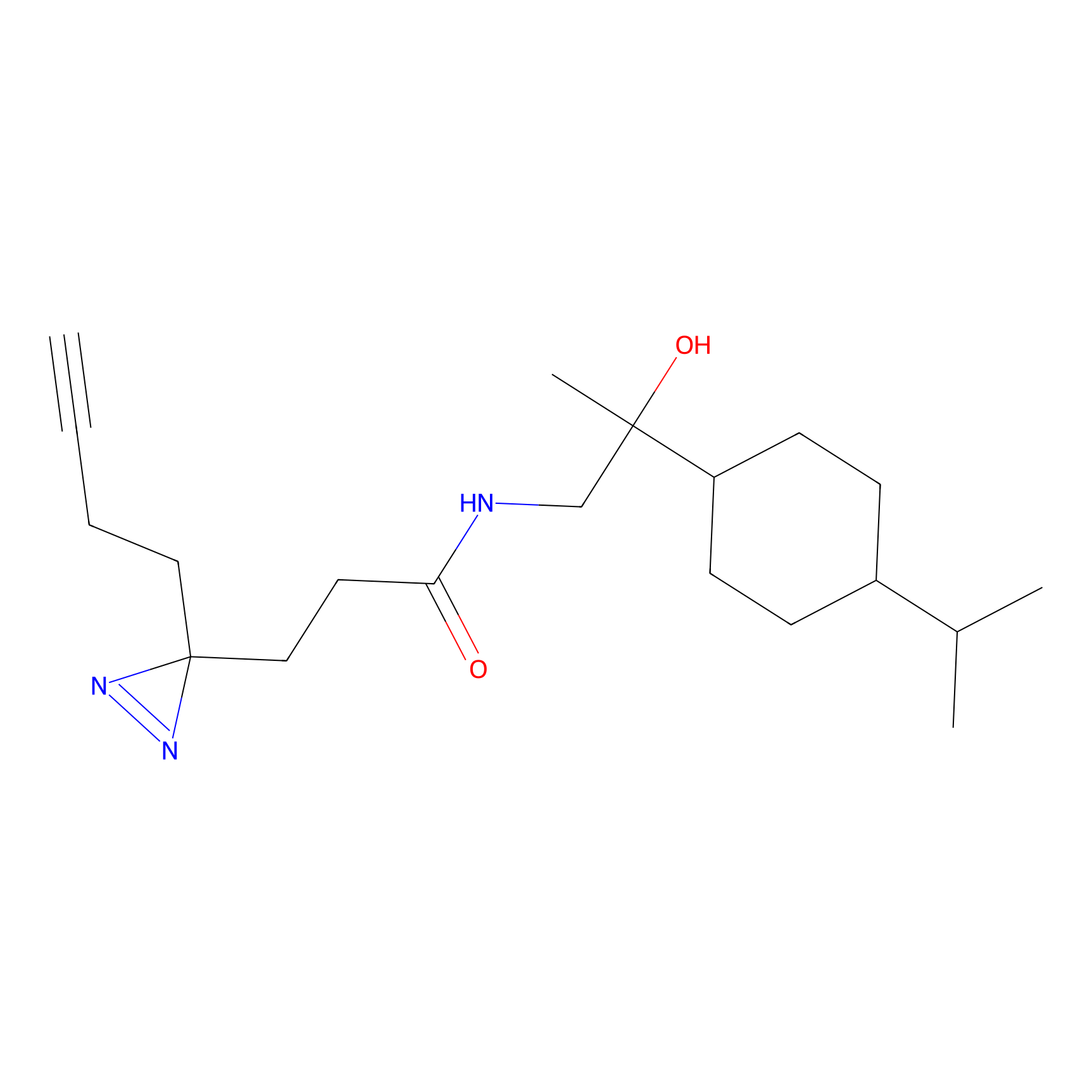
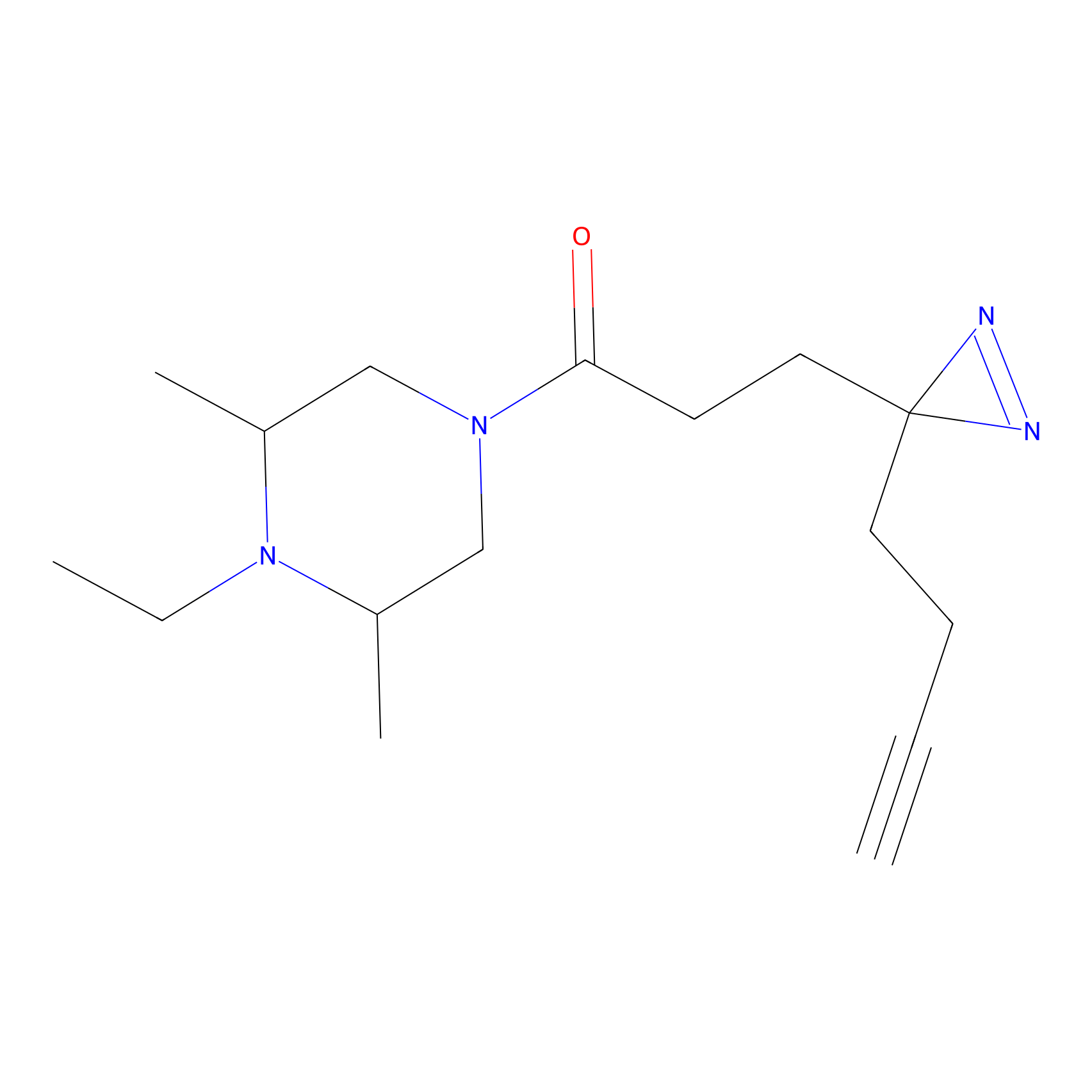
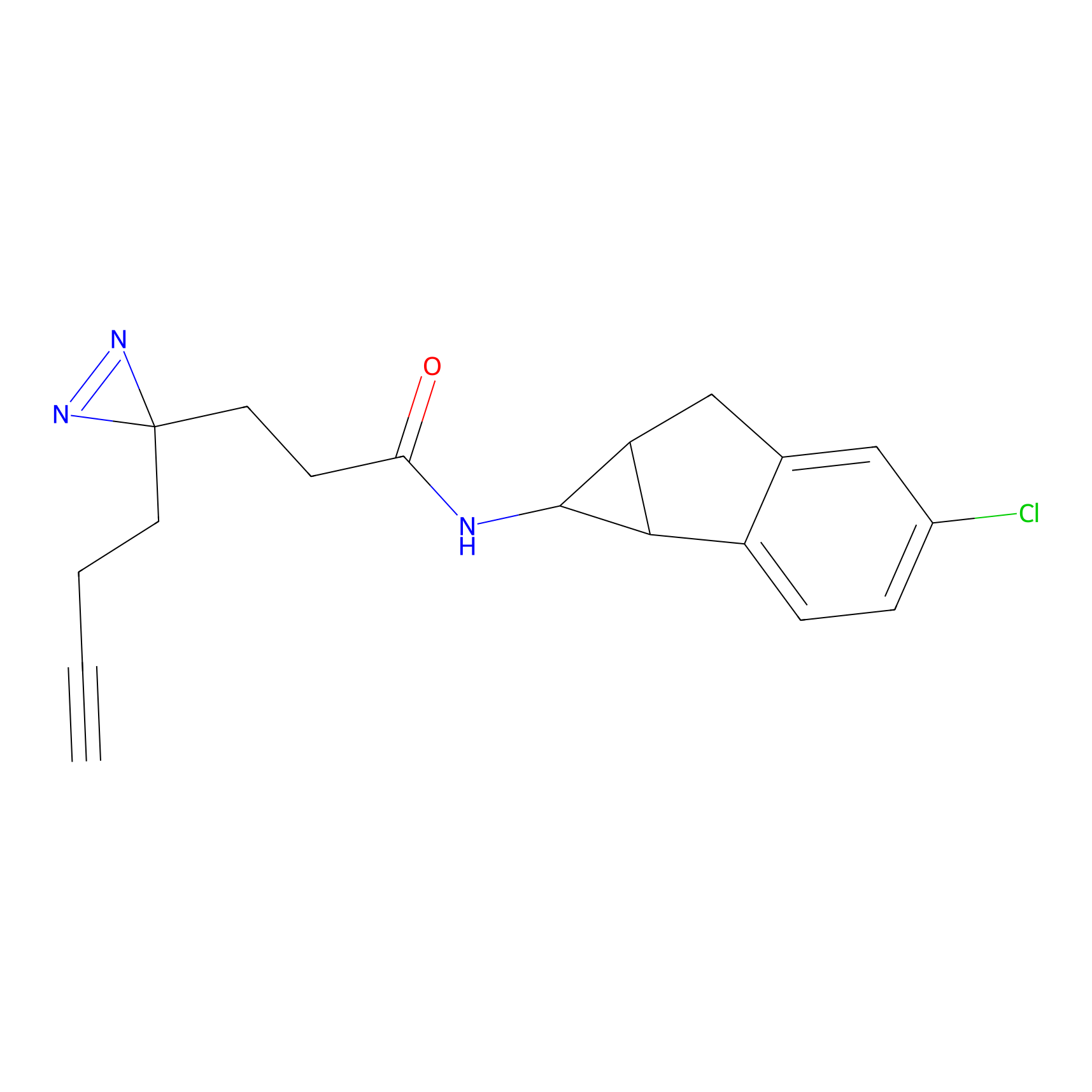
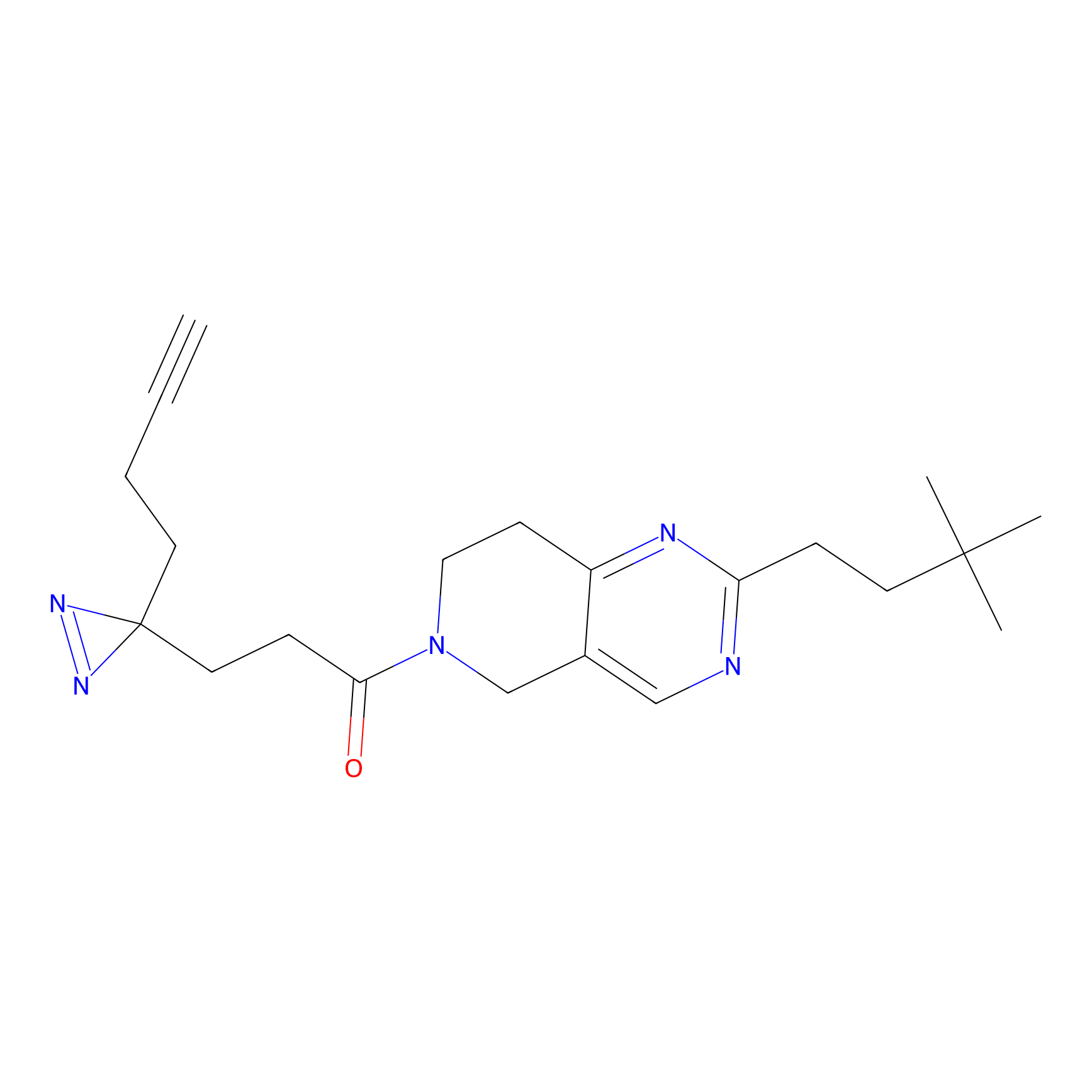
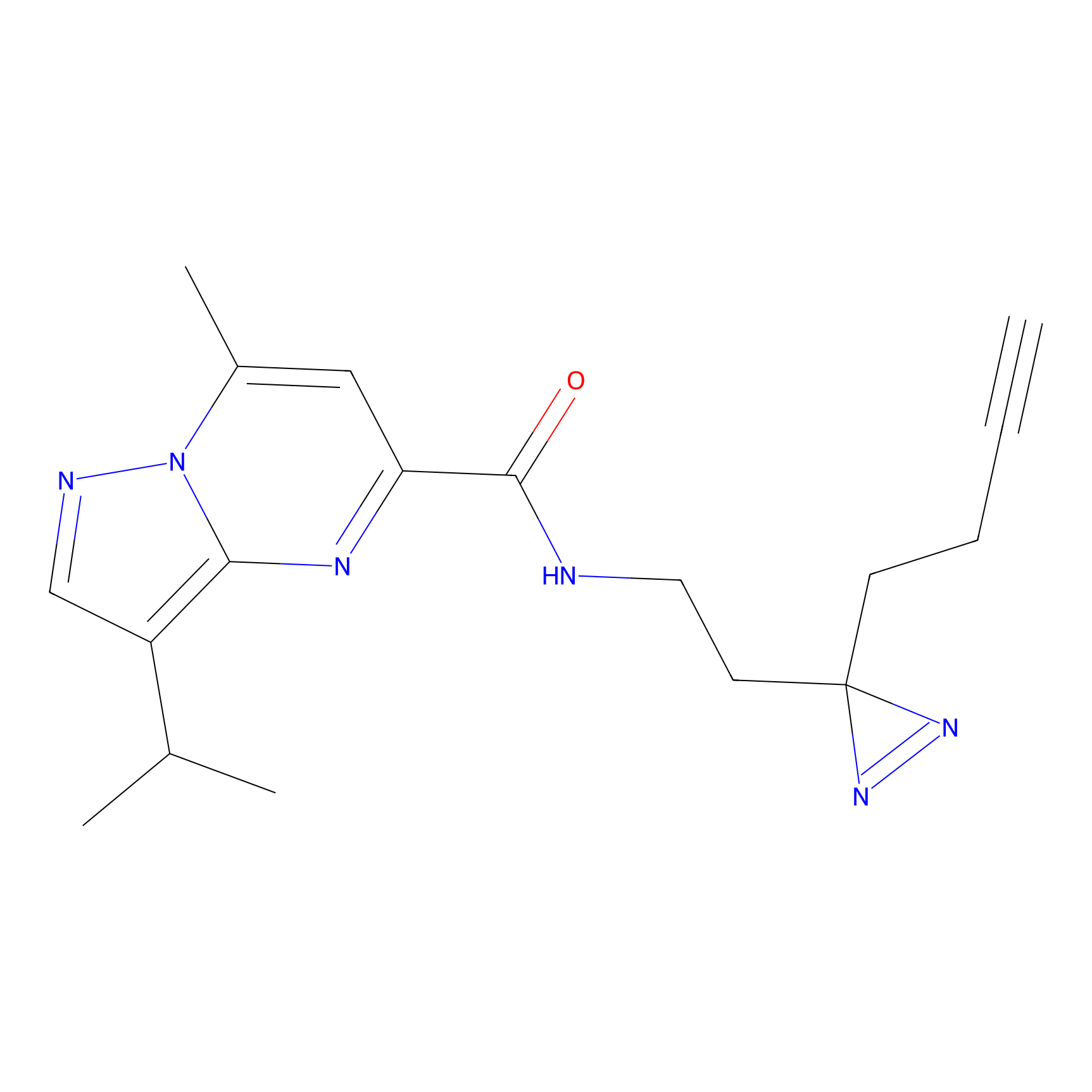
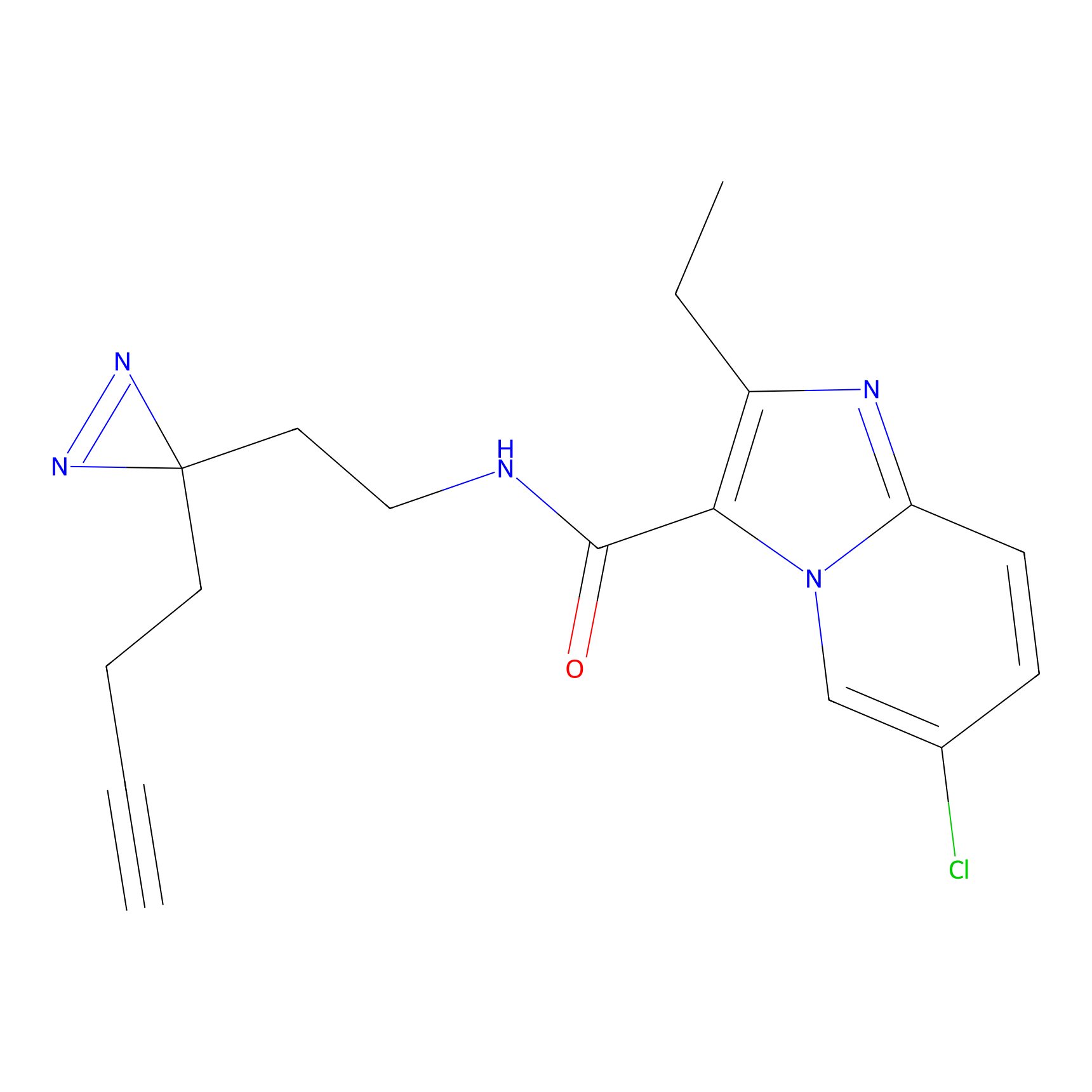
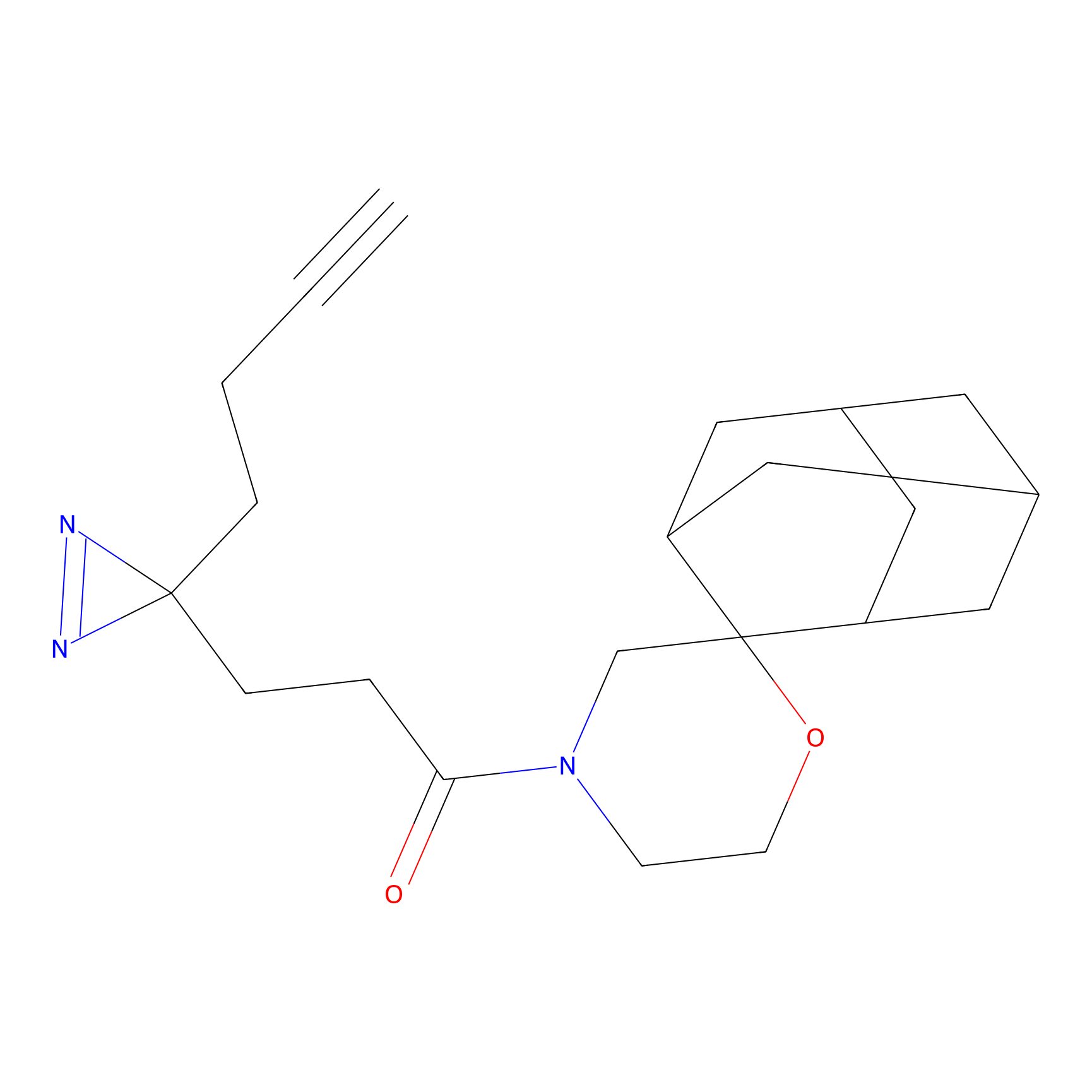
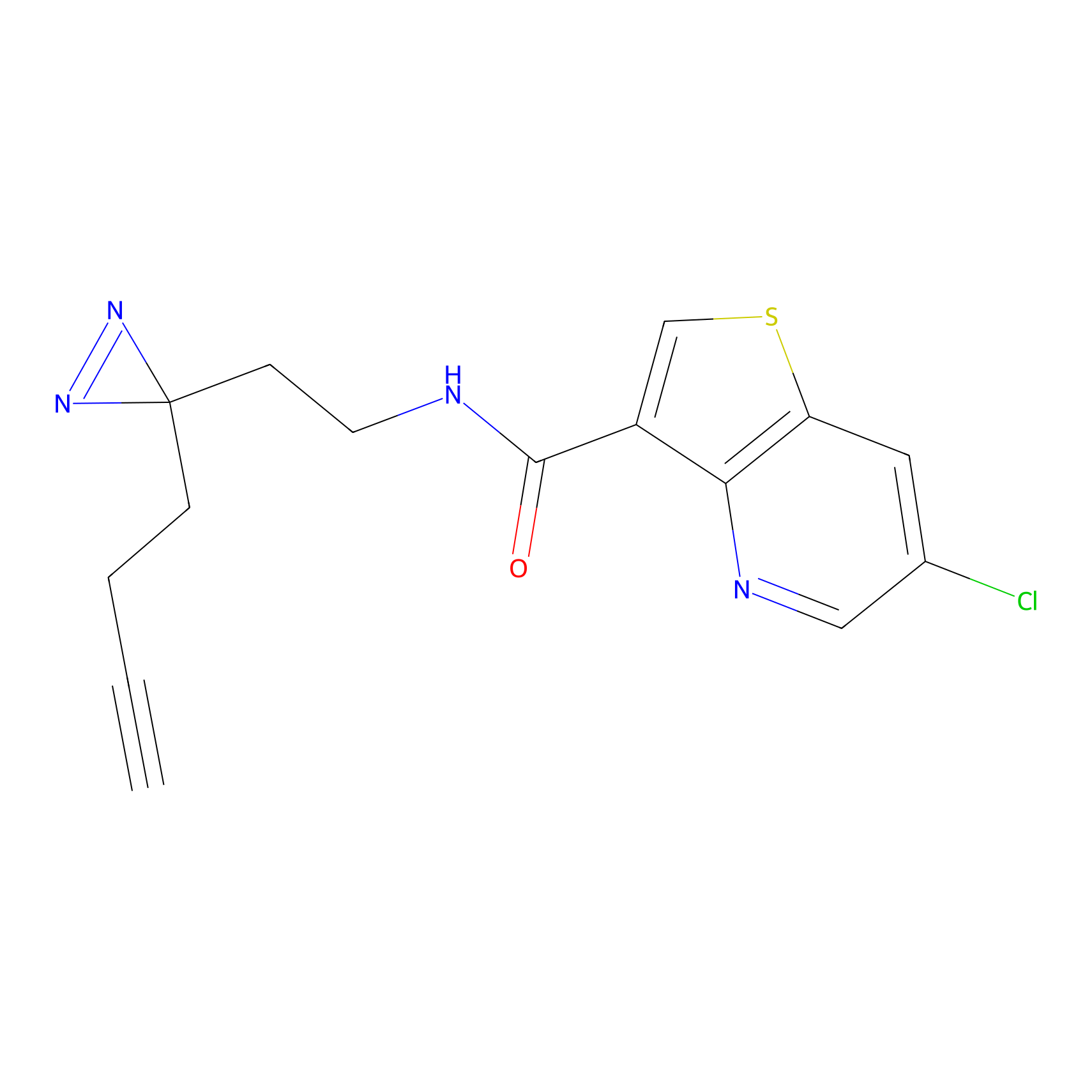
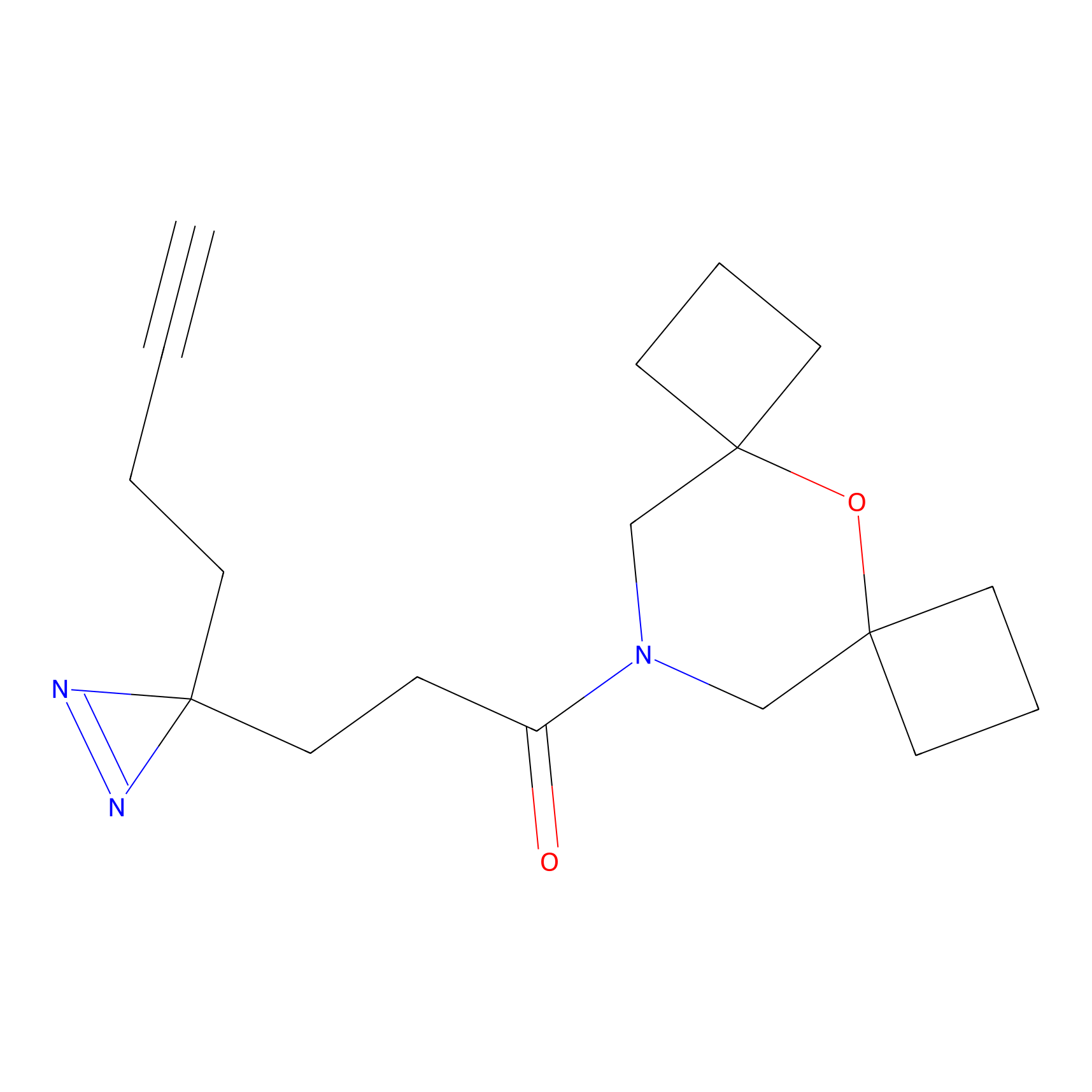
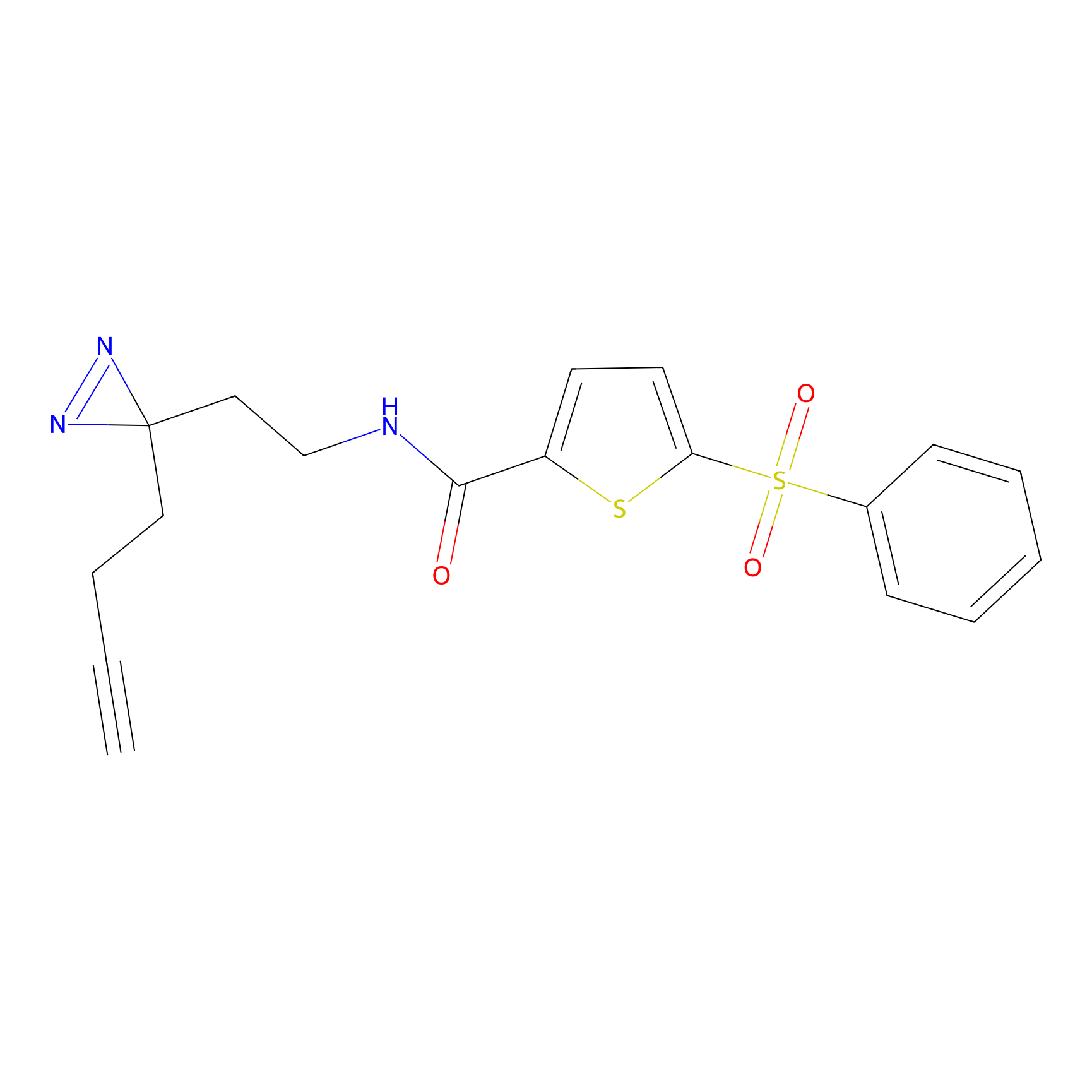
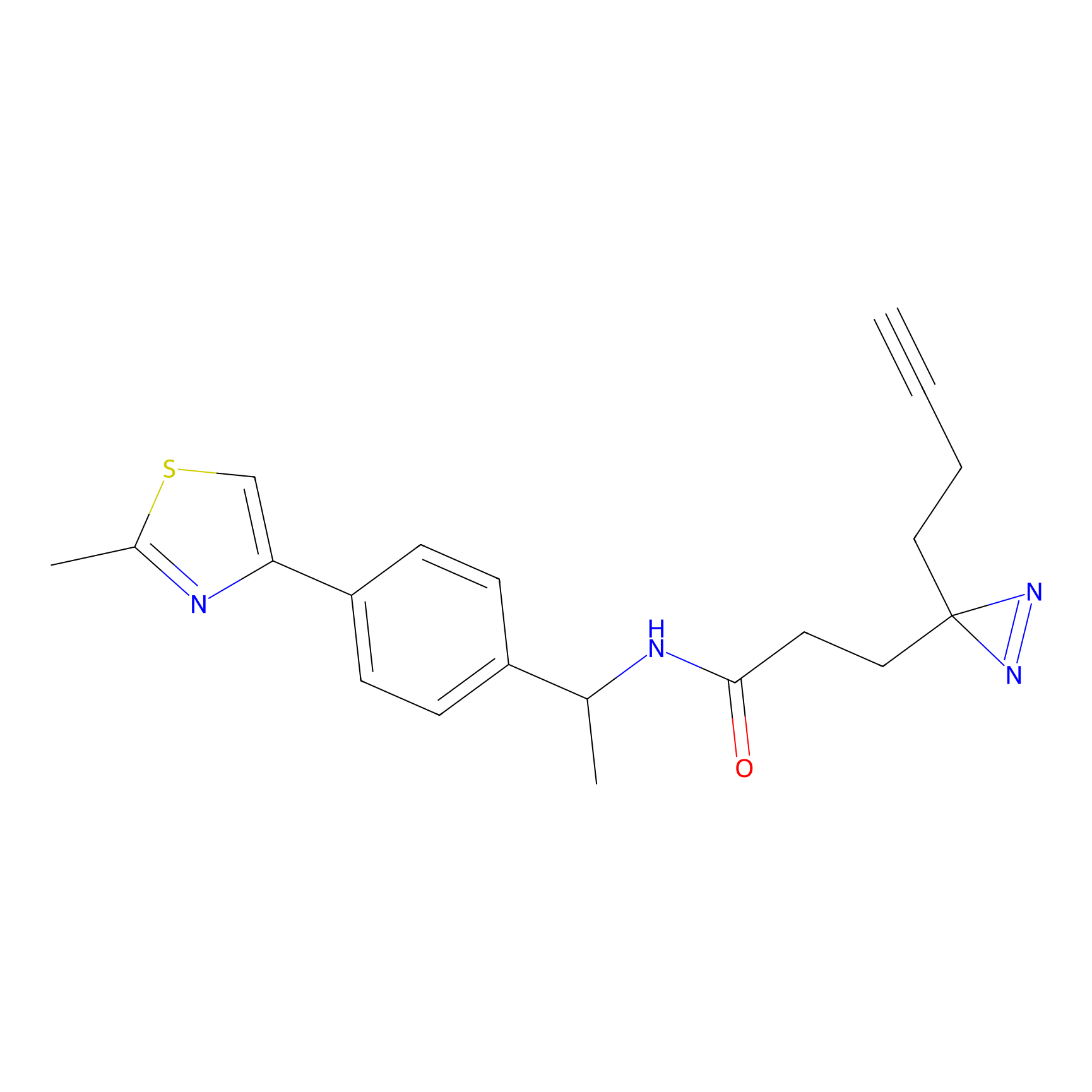
DBIA Probe Info |
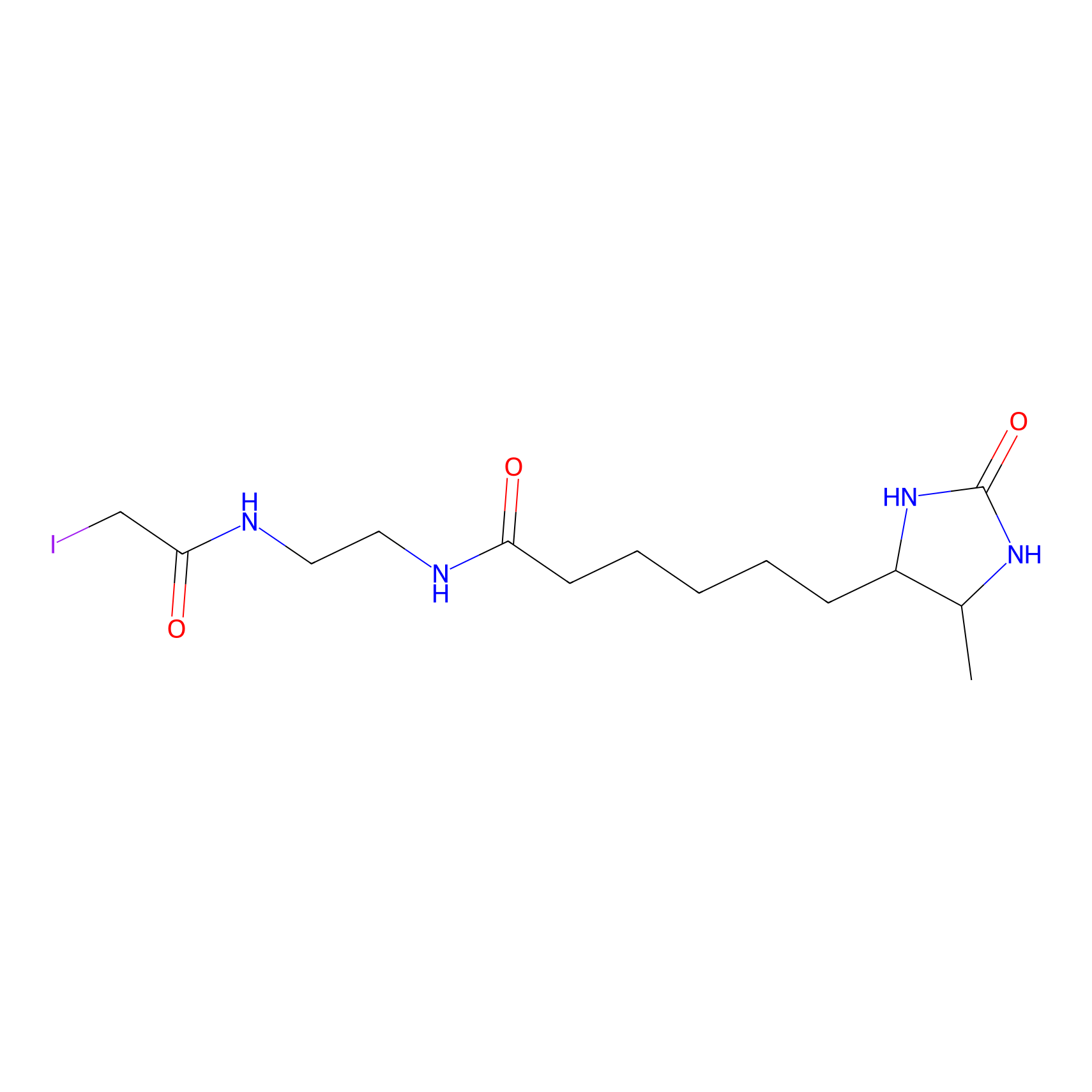 |
C296(1.14) | LDD1509 | [3] | |
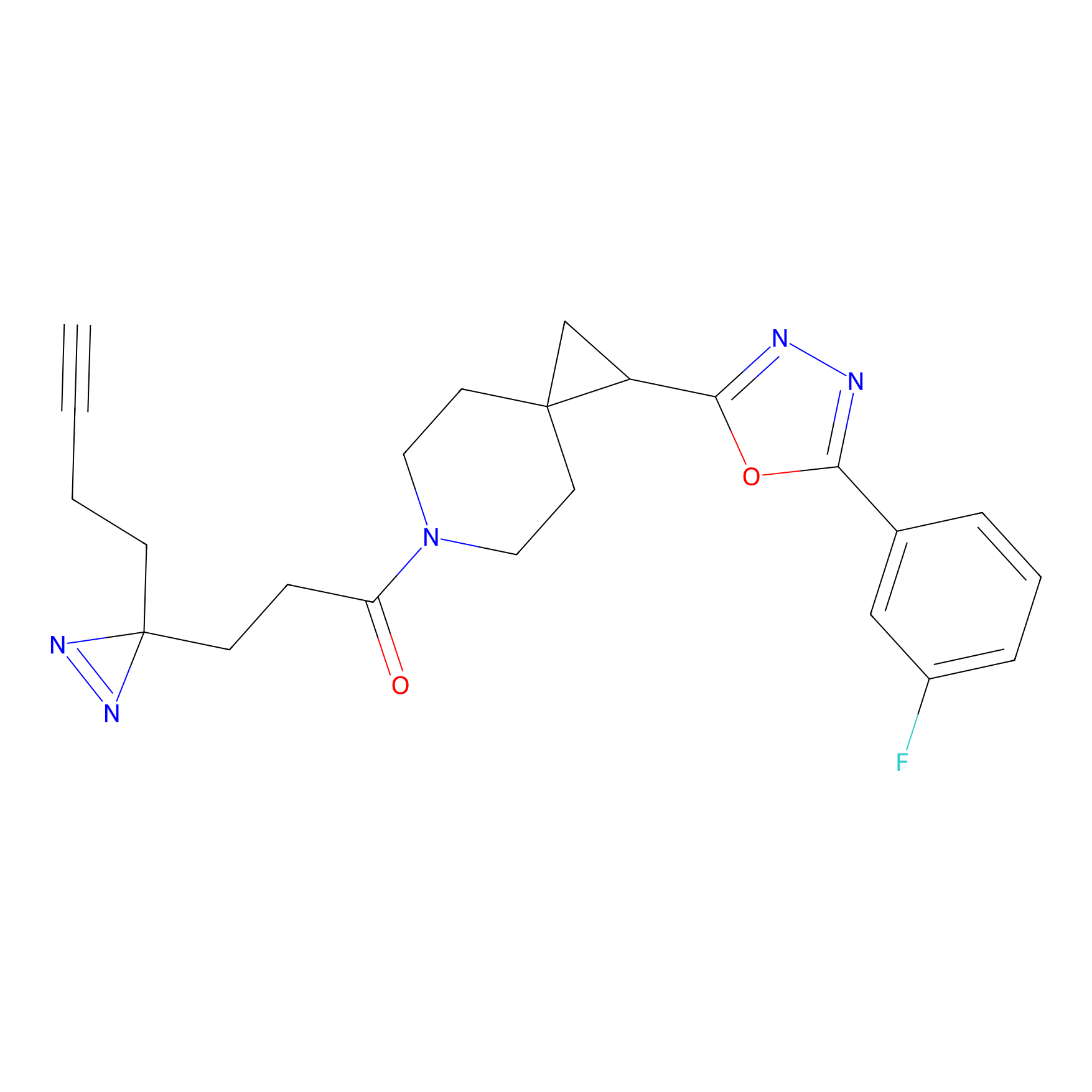
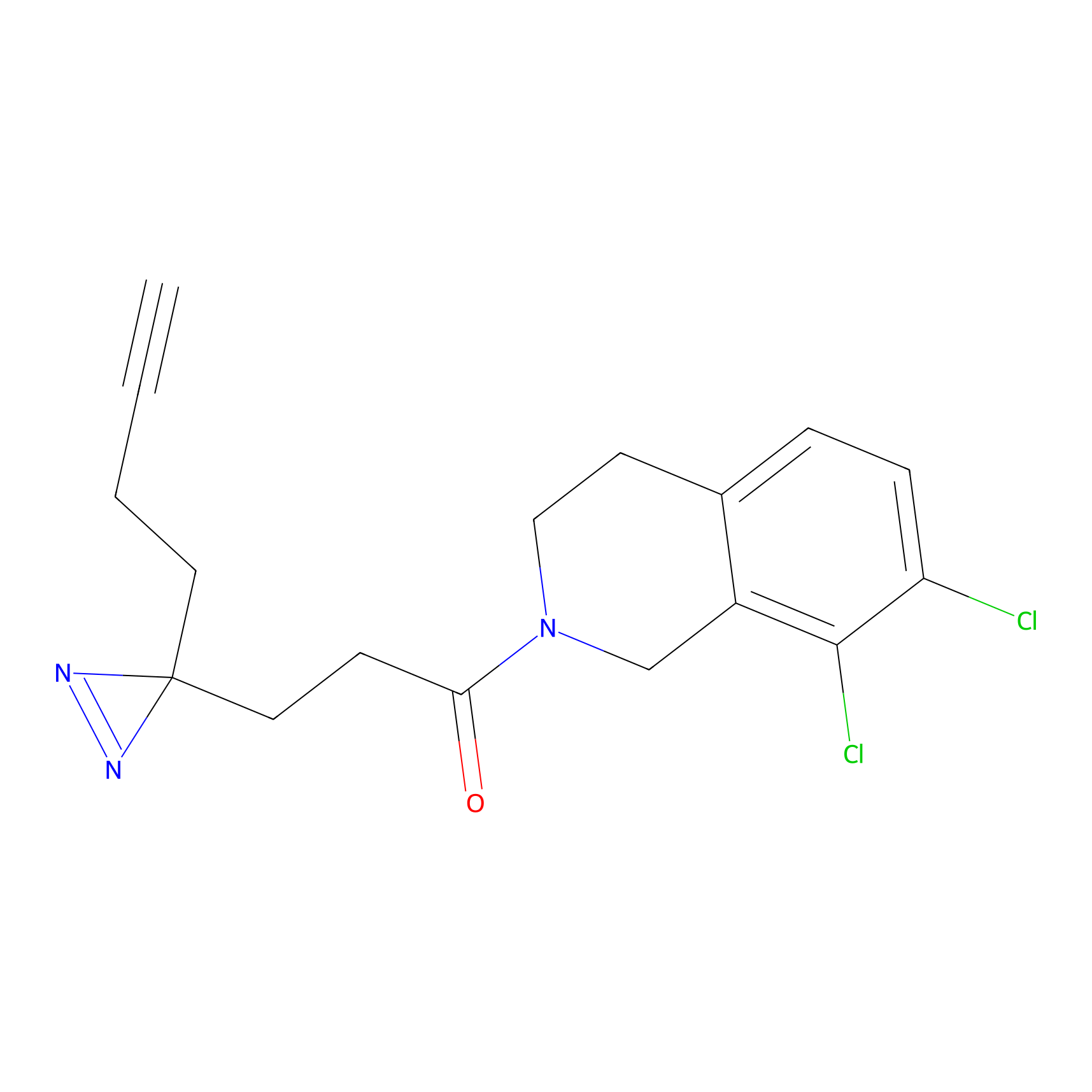
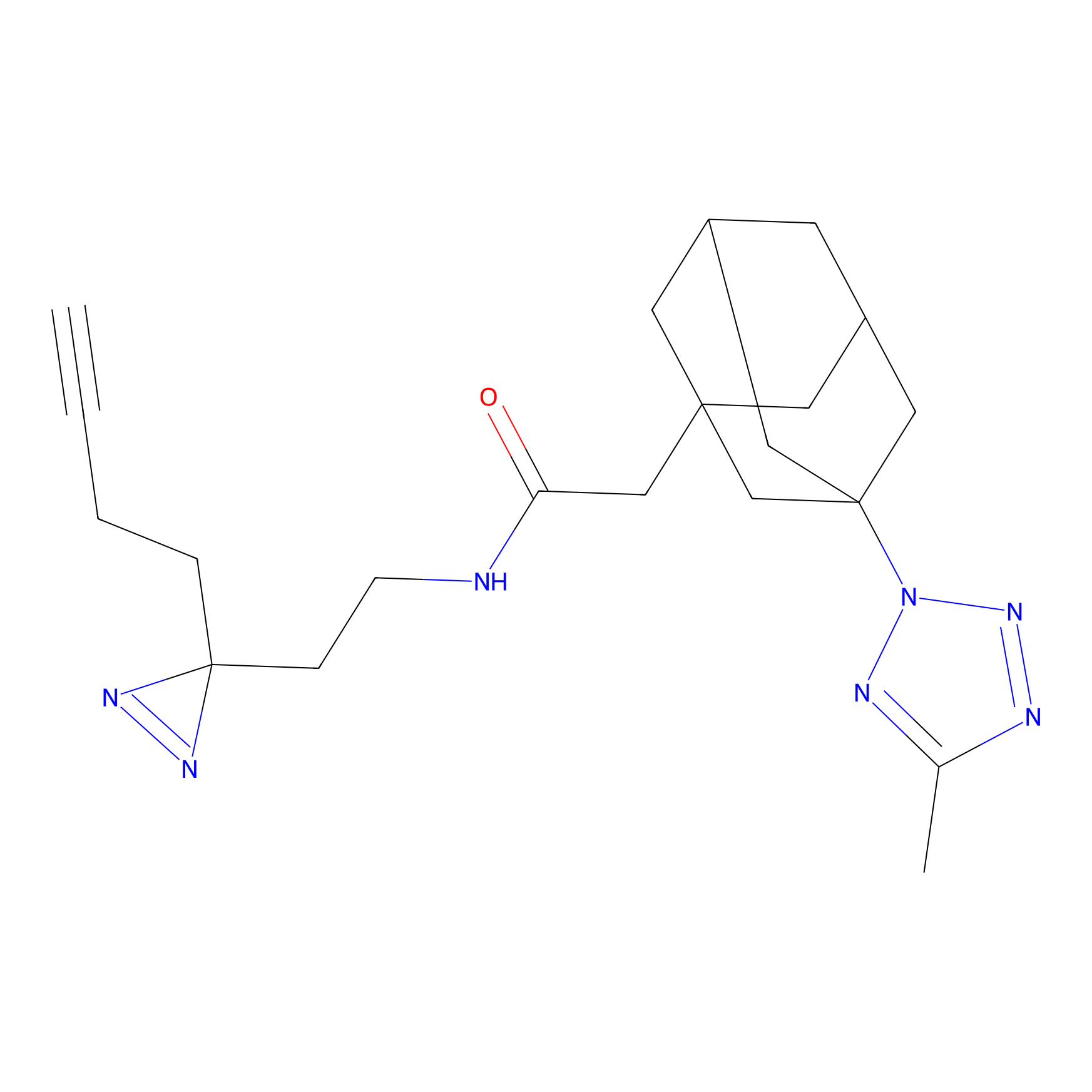
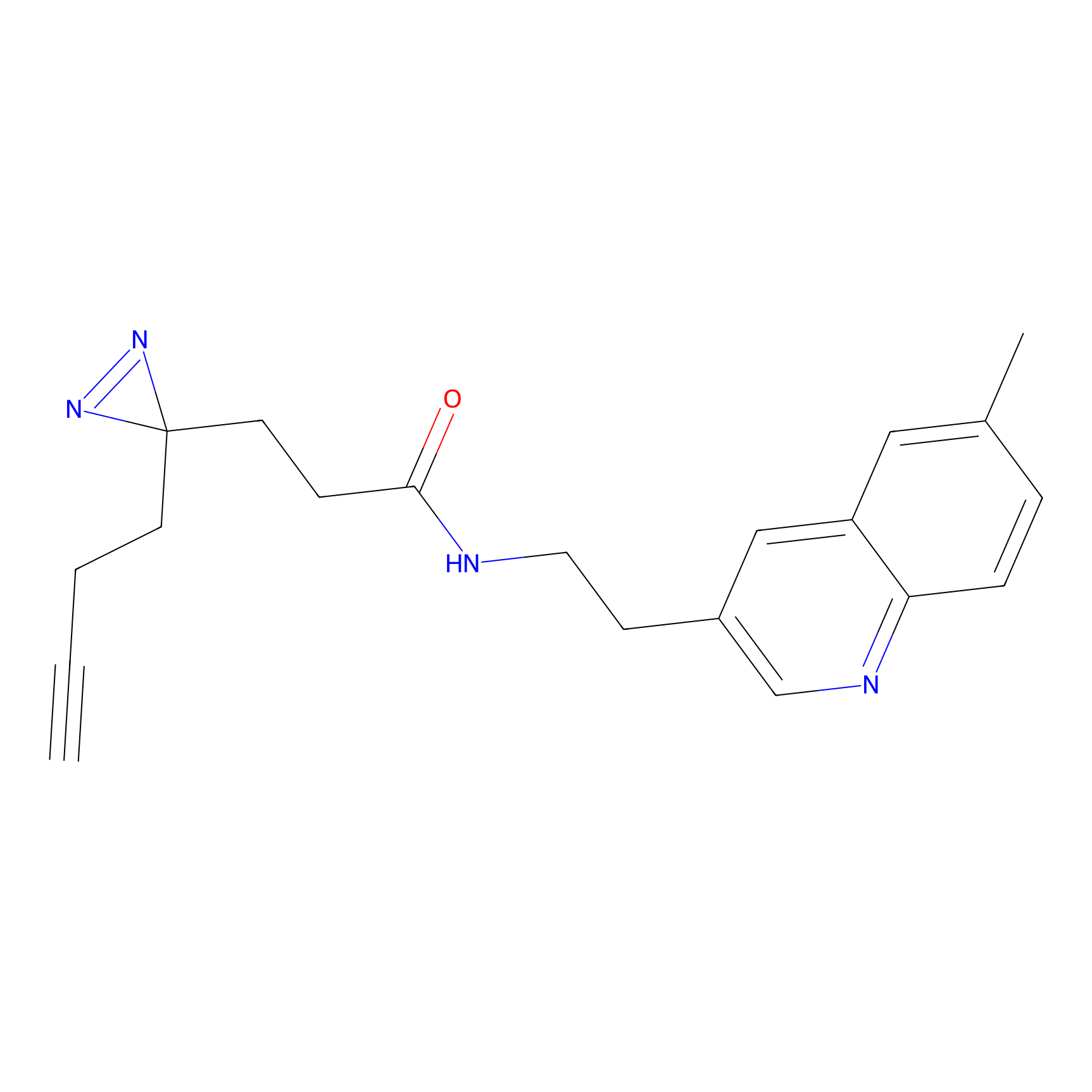
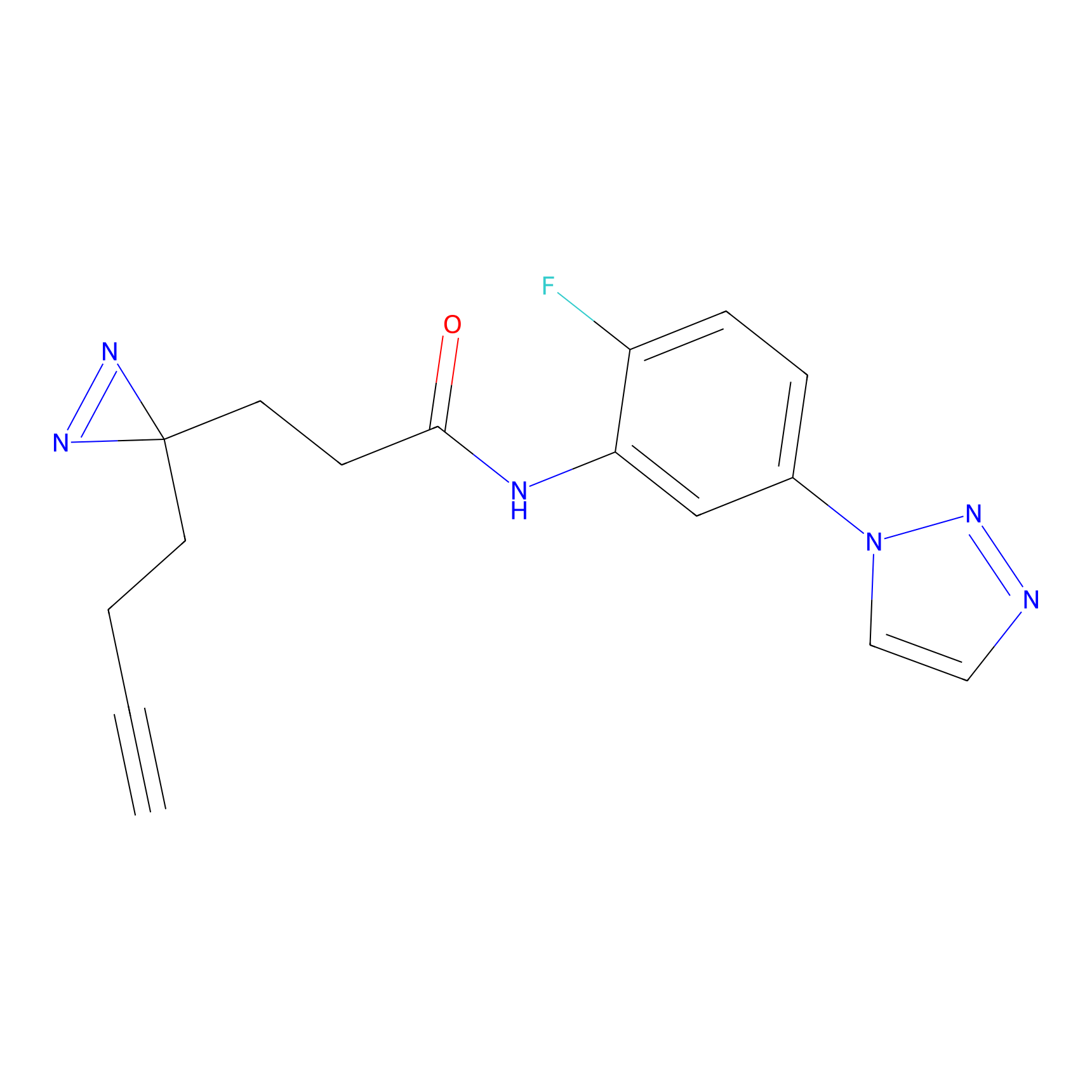
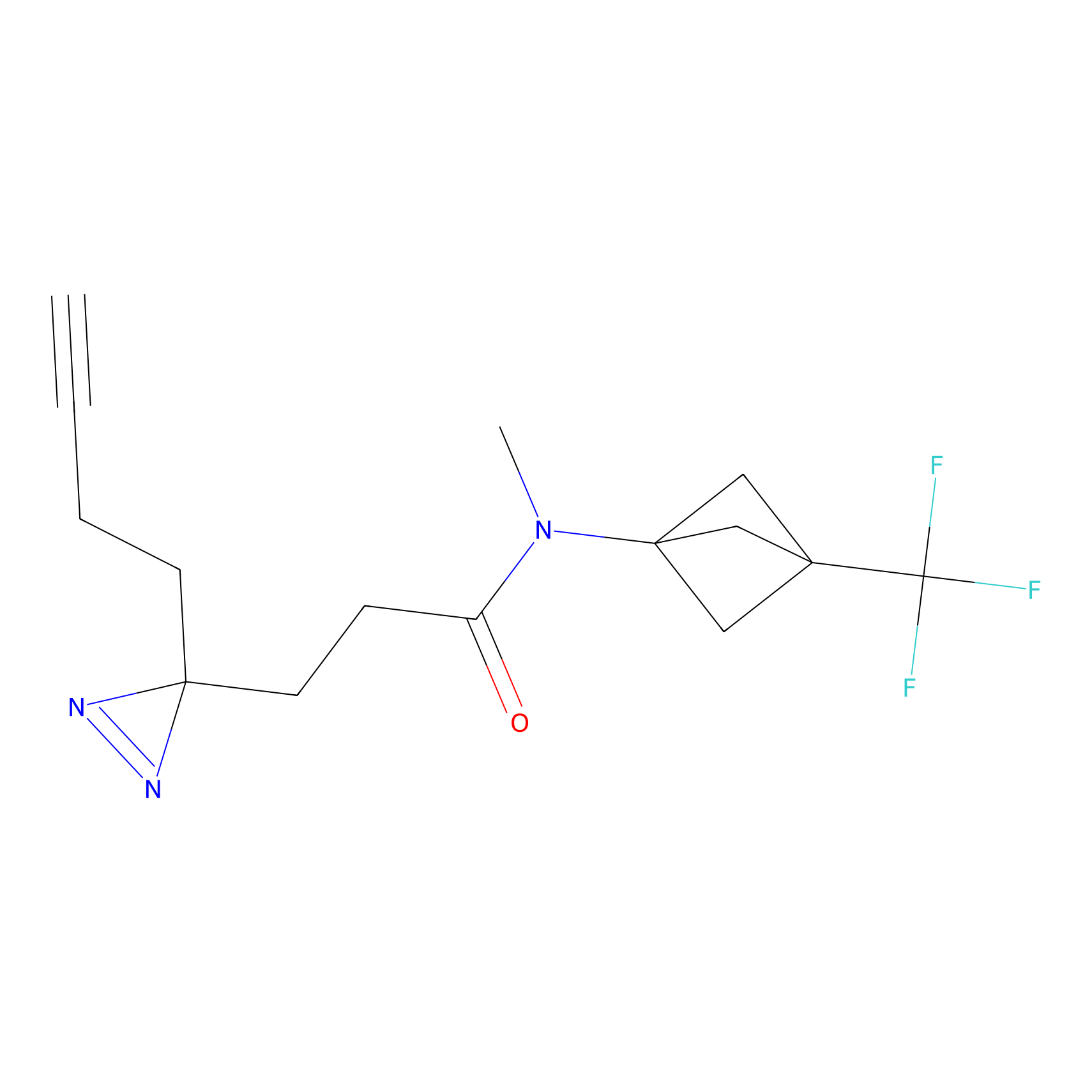
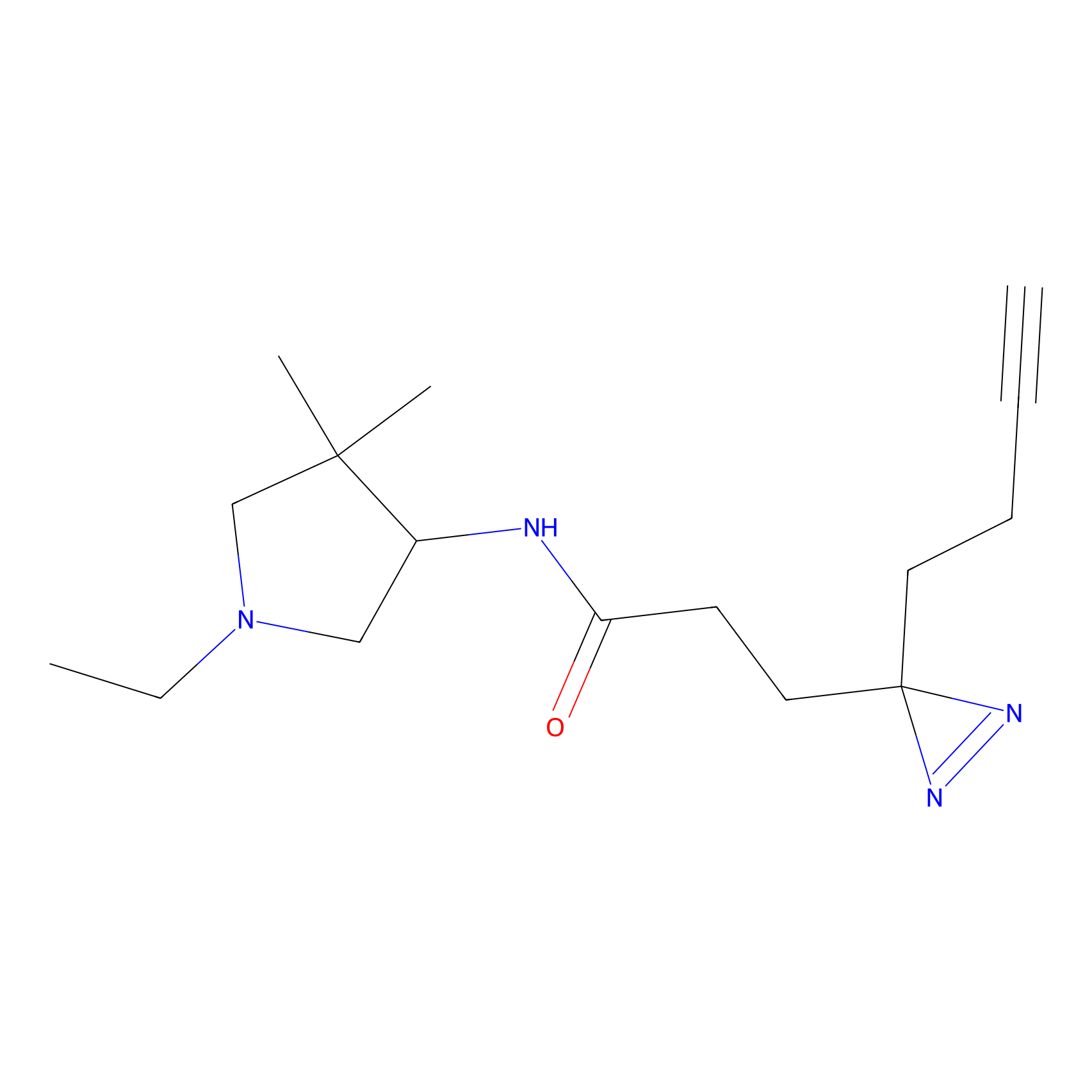
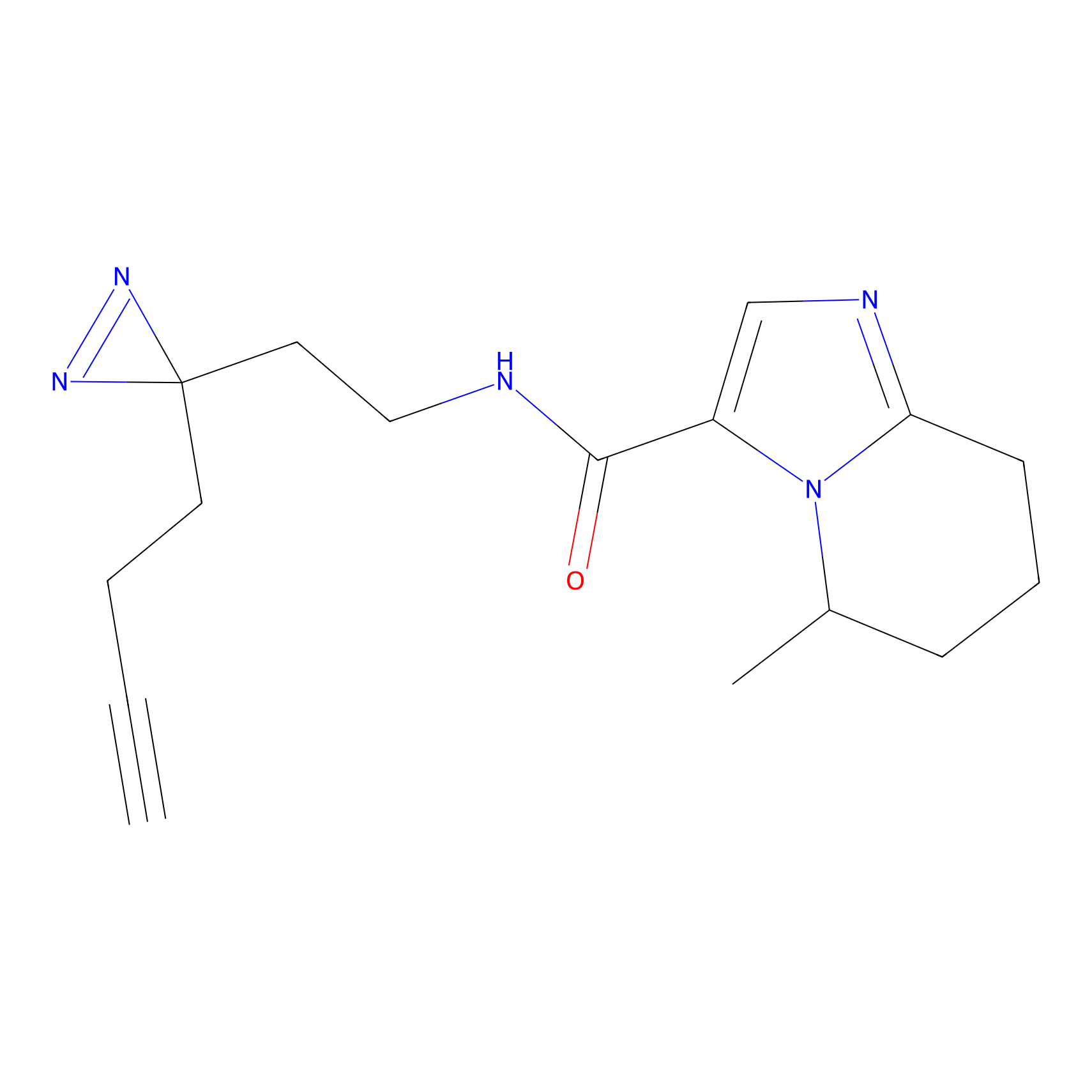
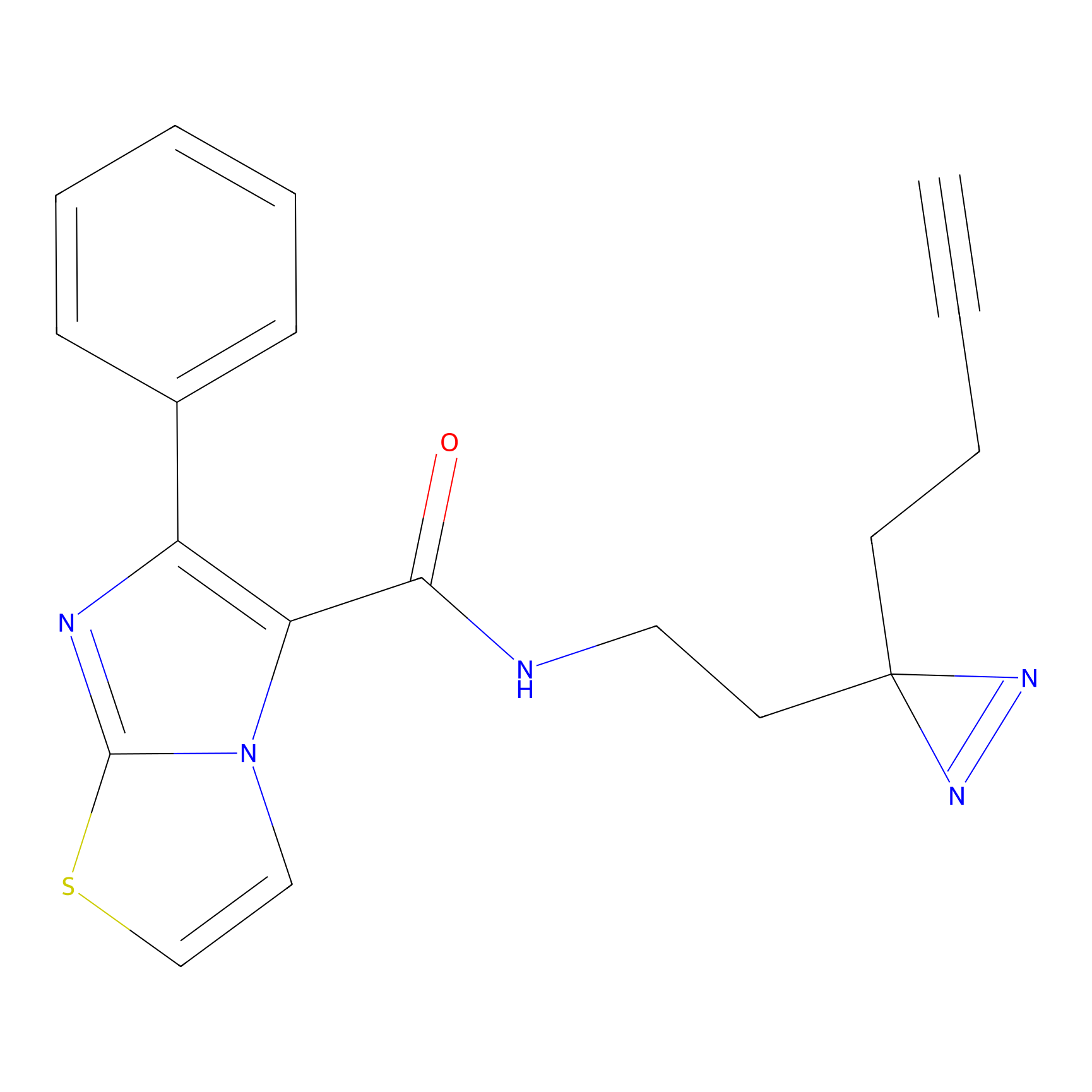
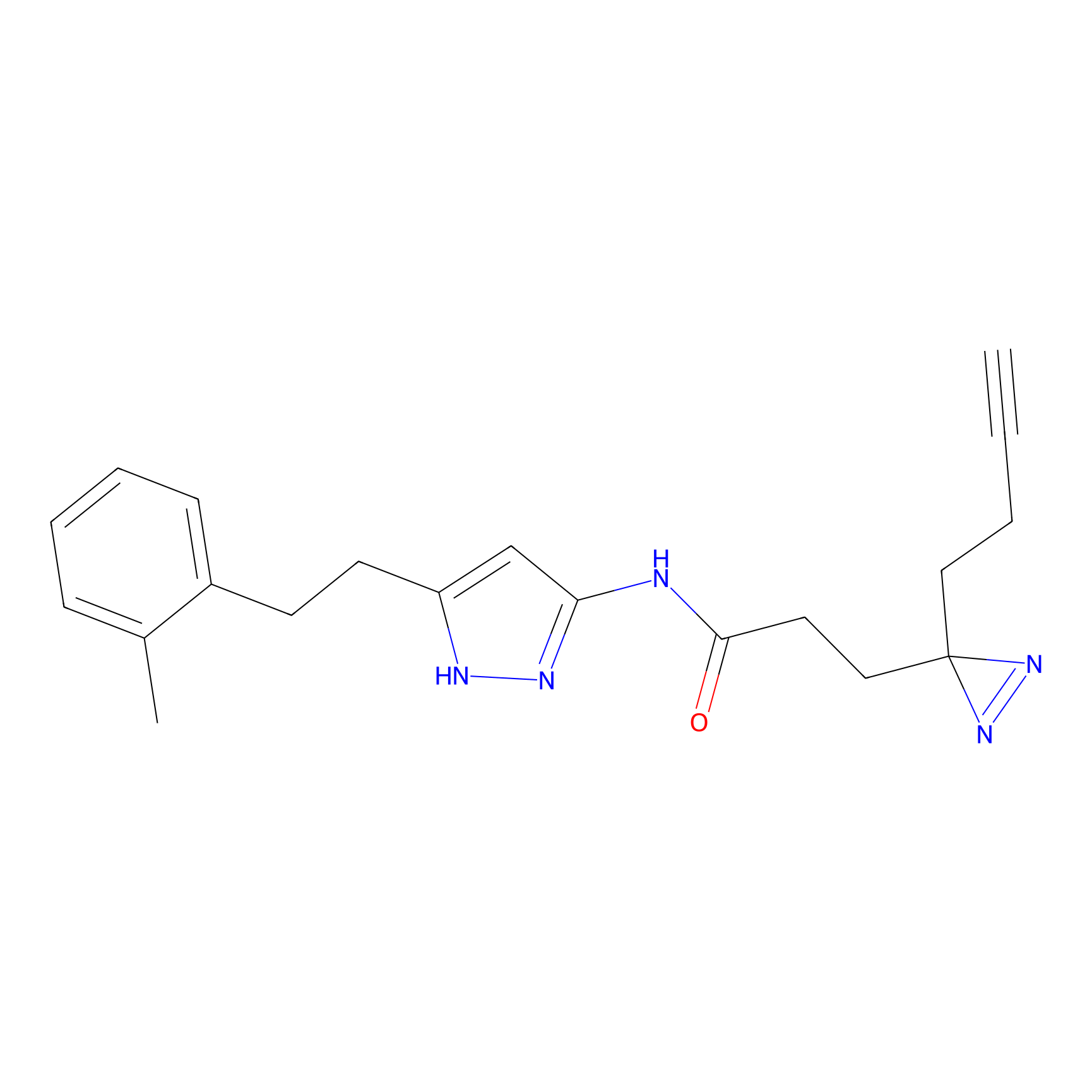
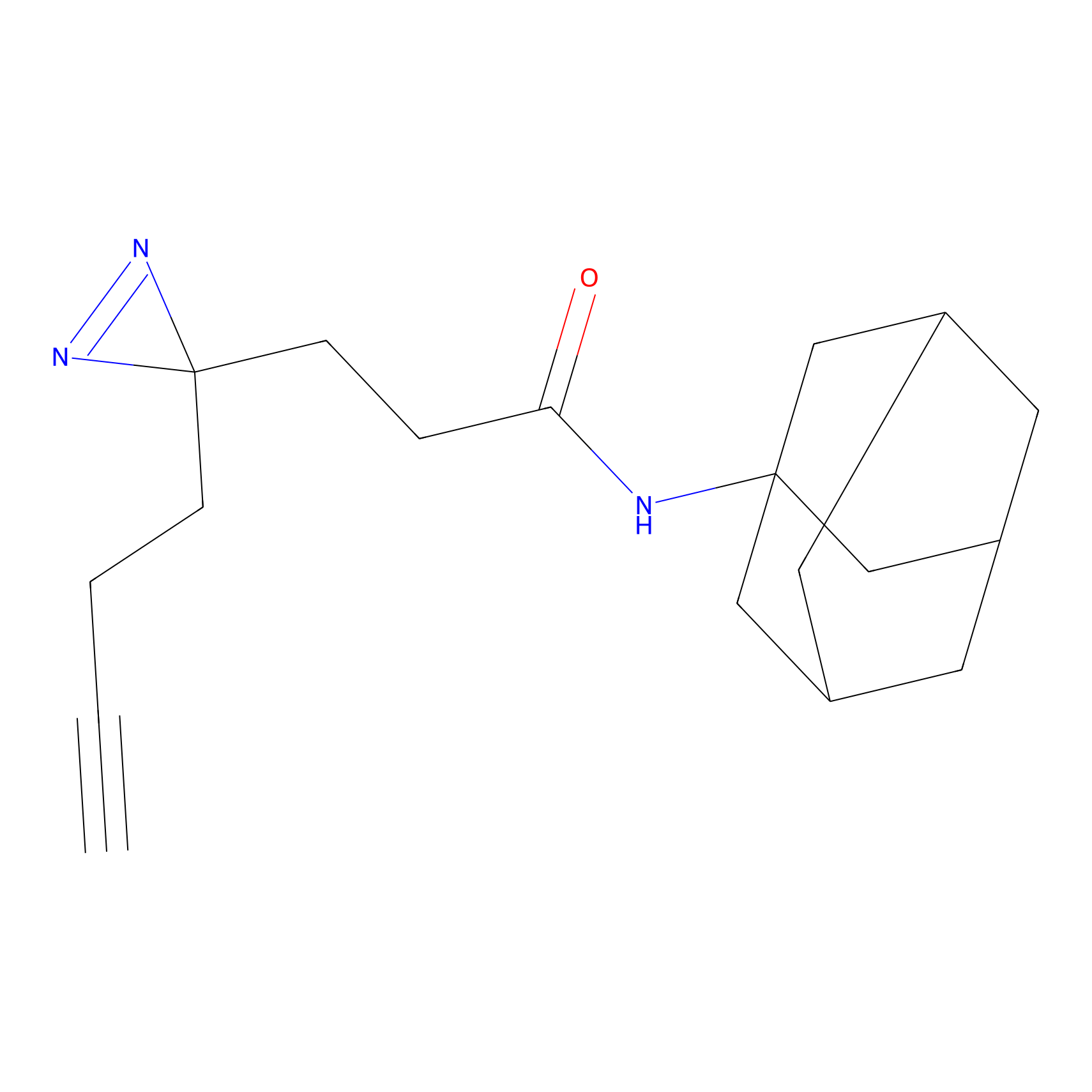
|
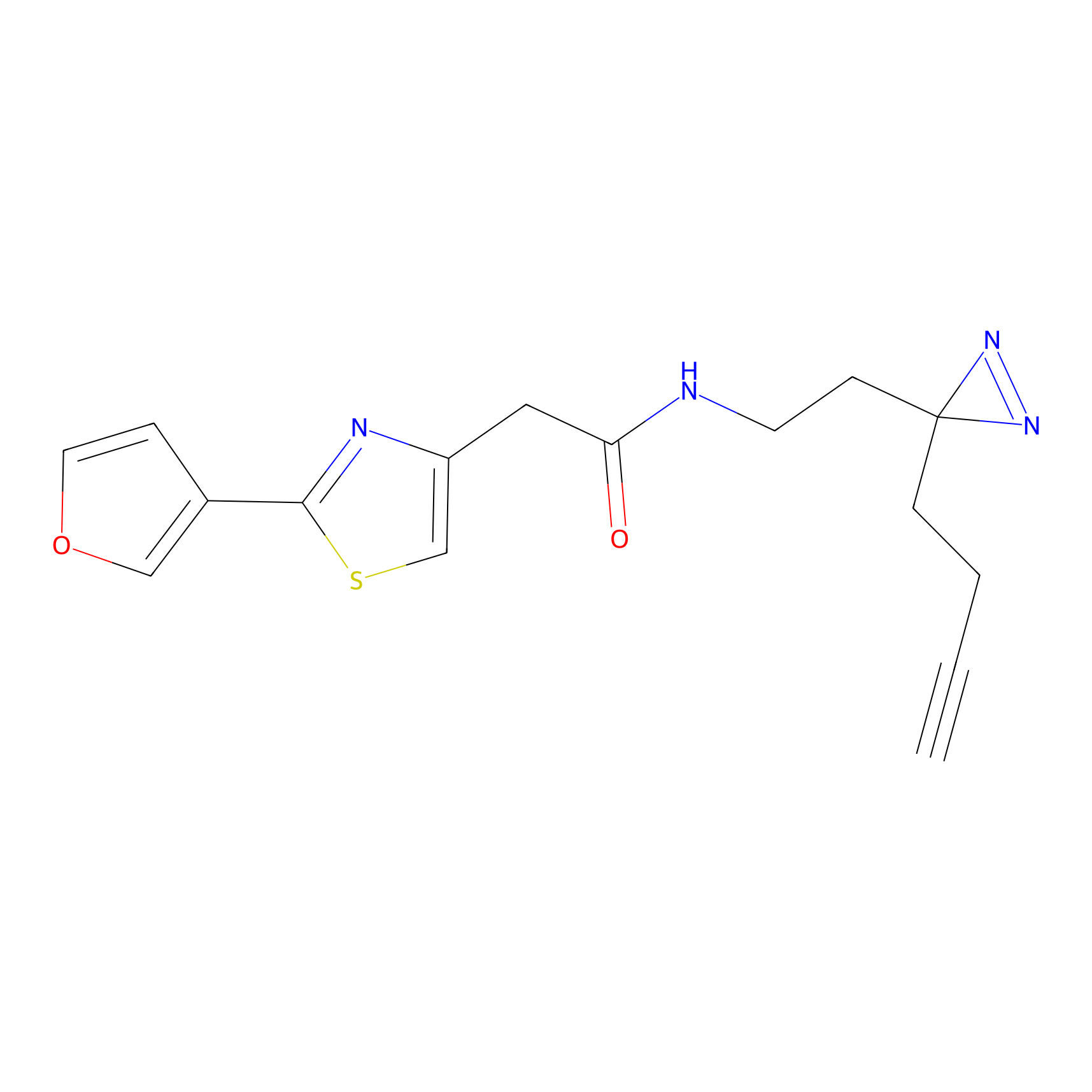
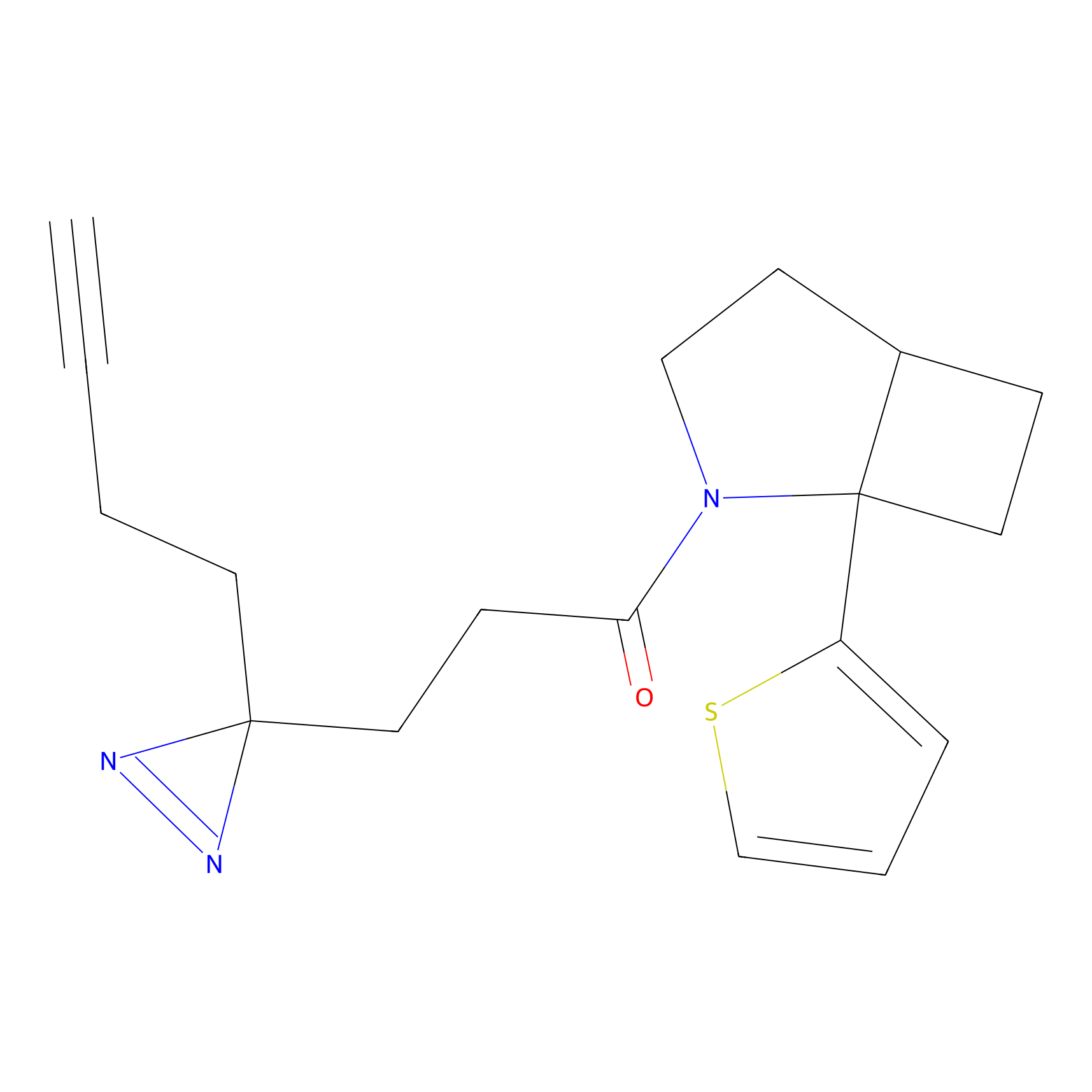
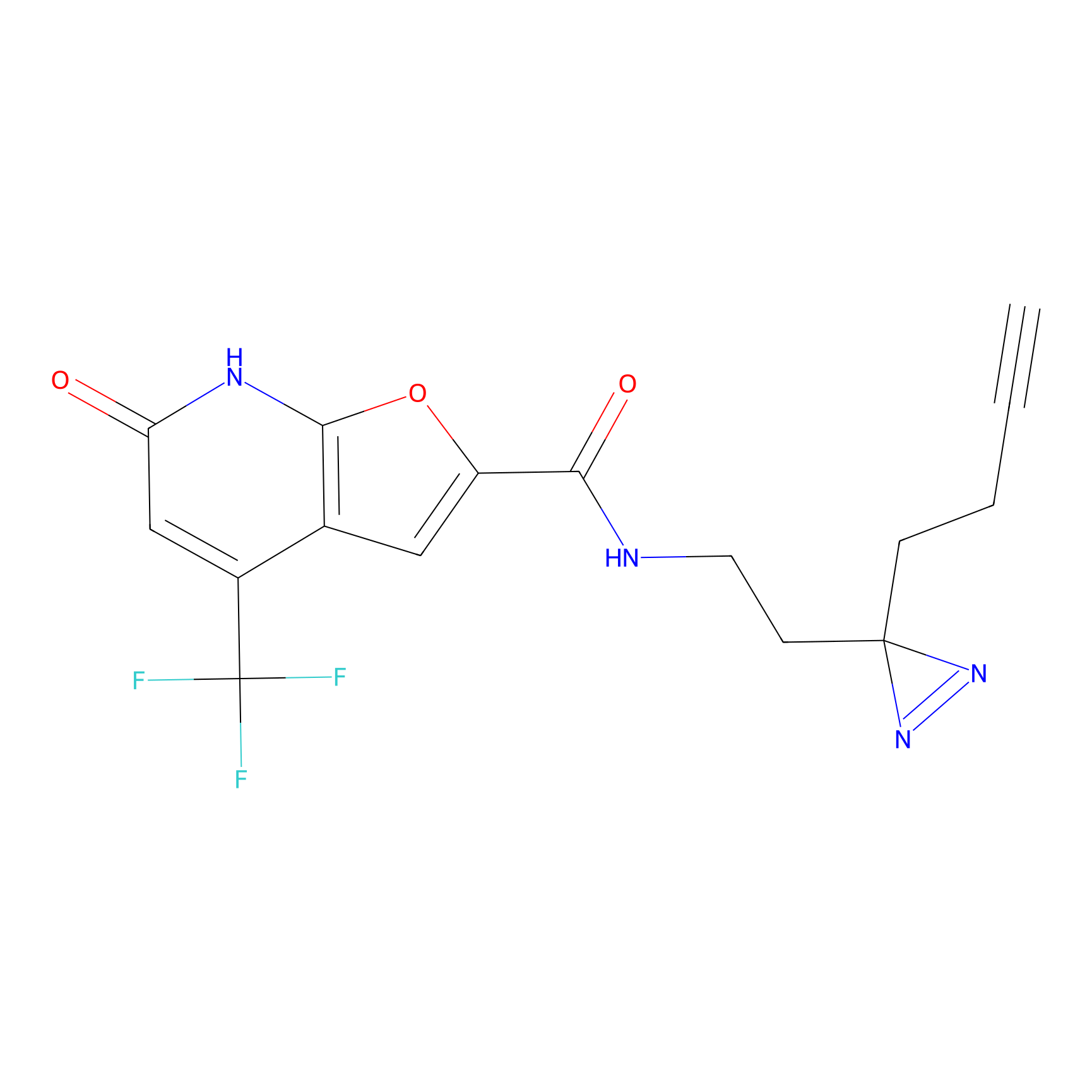
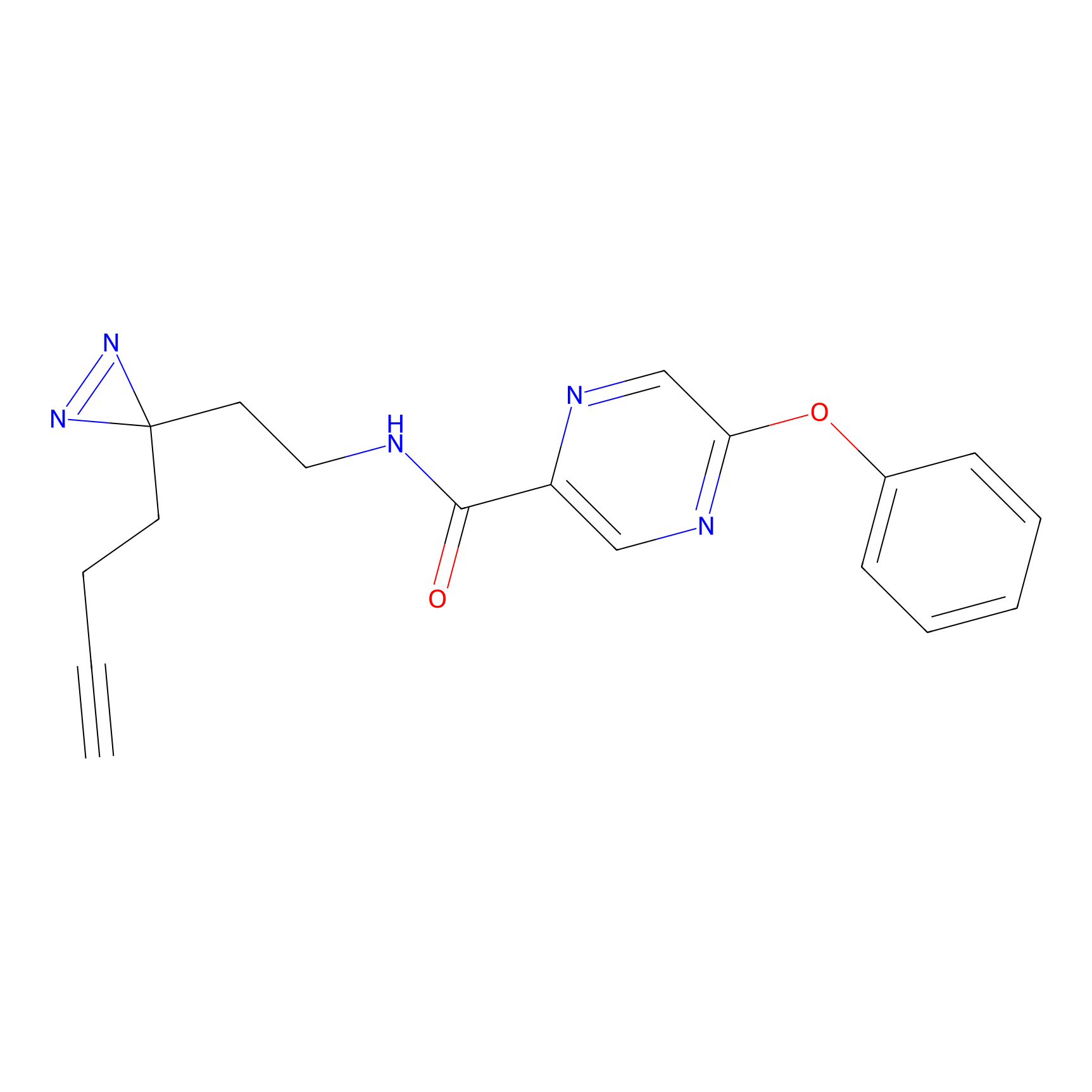
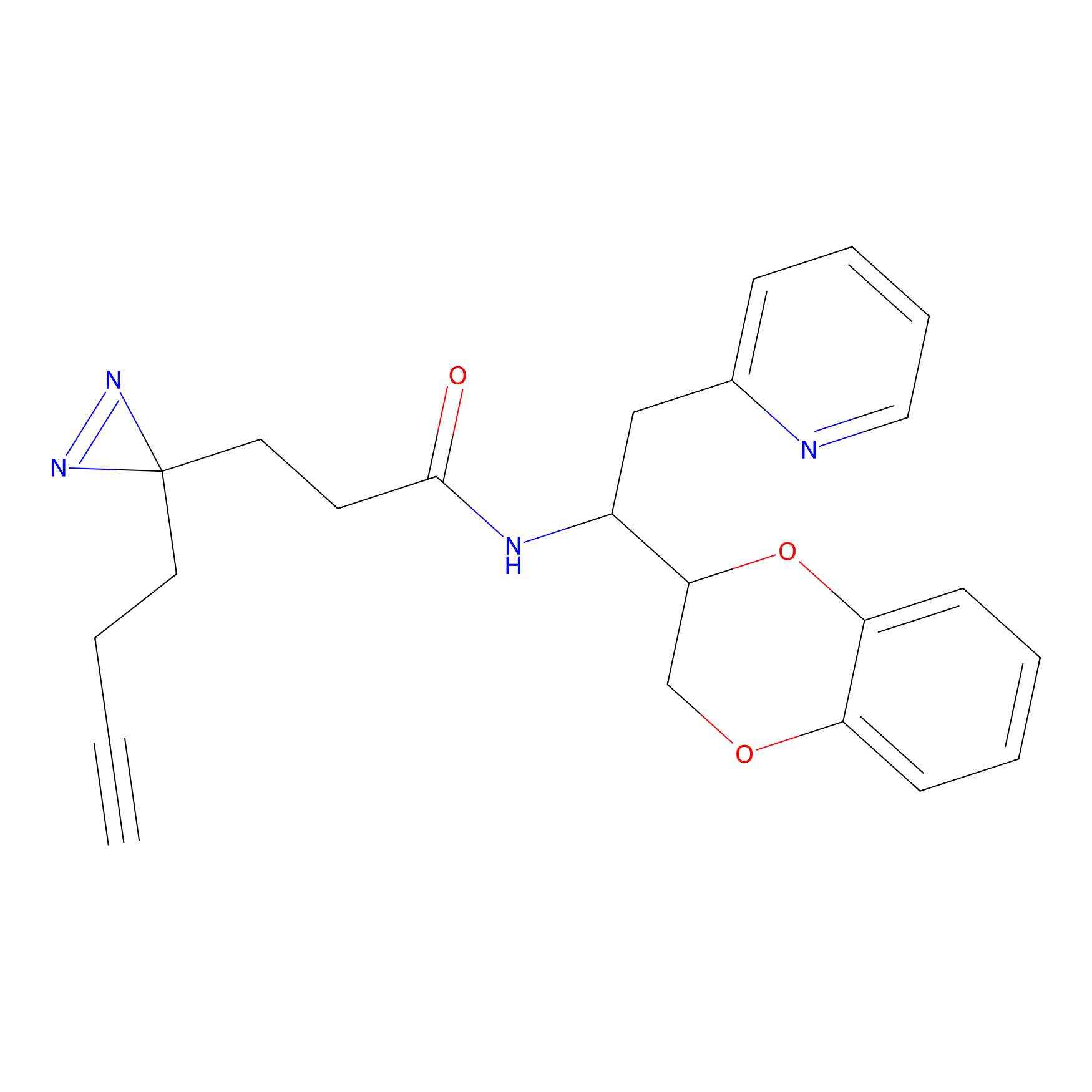
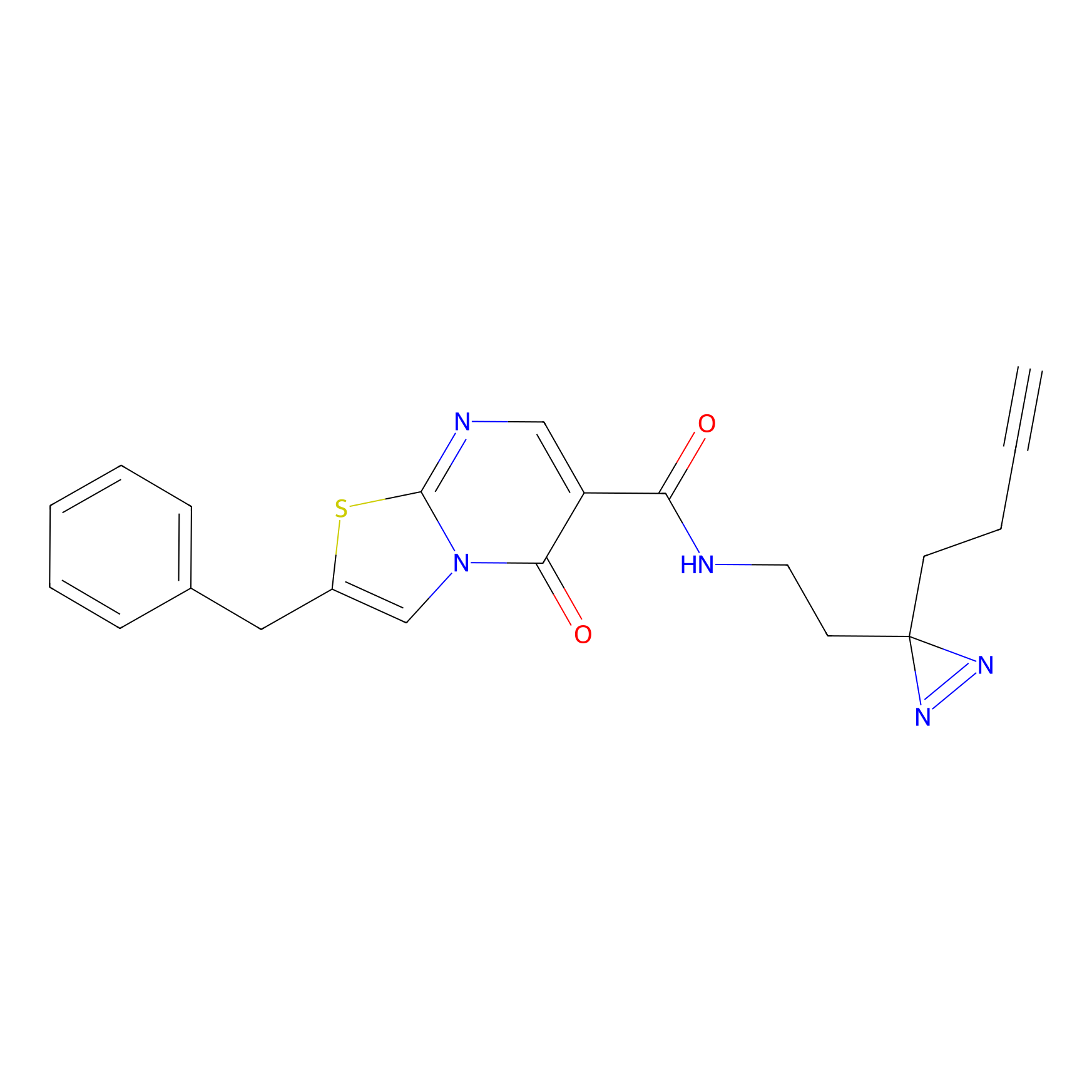
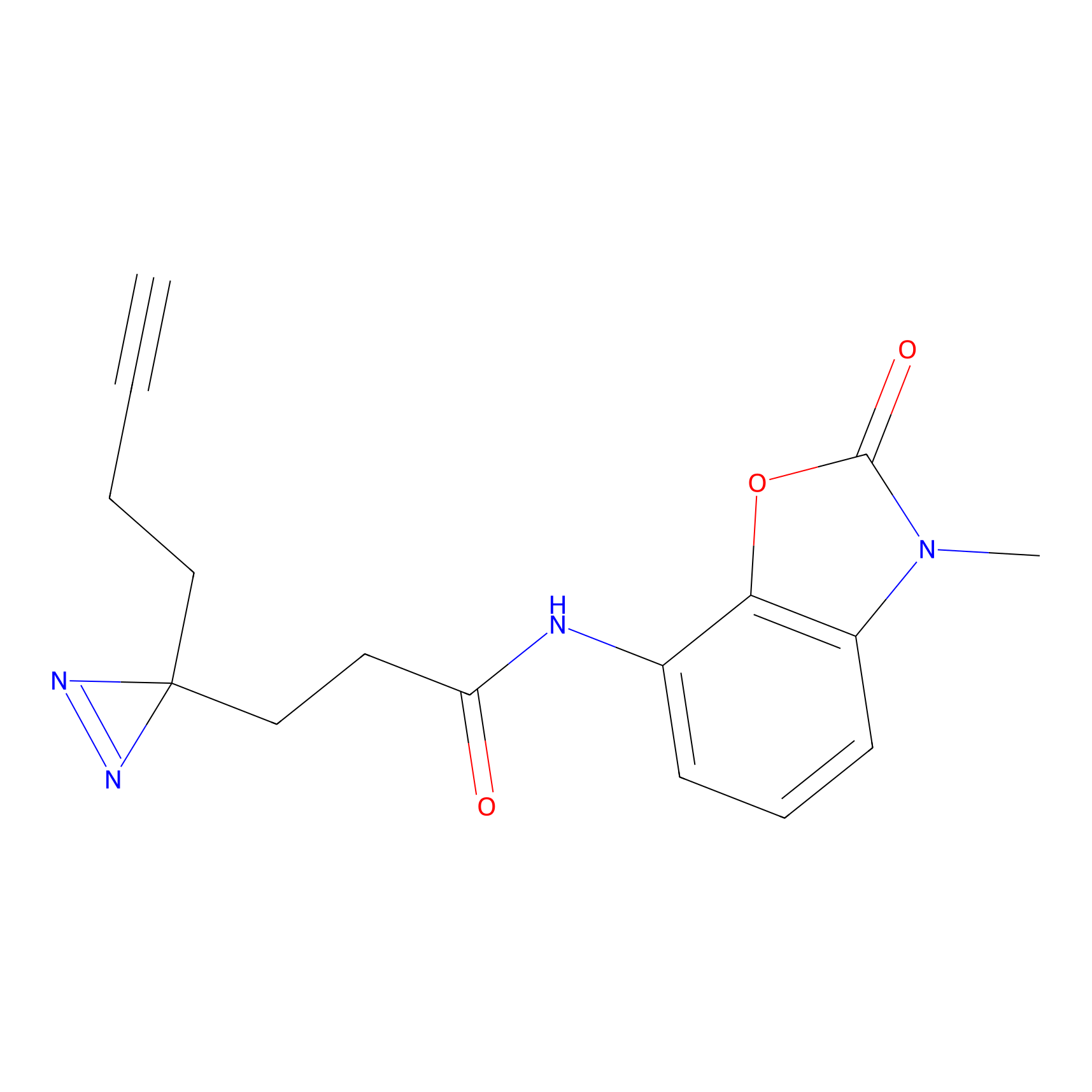
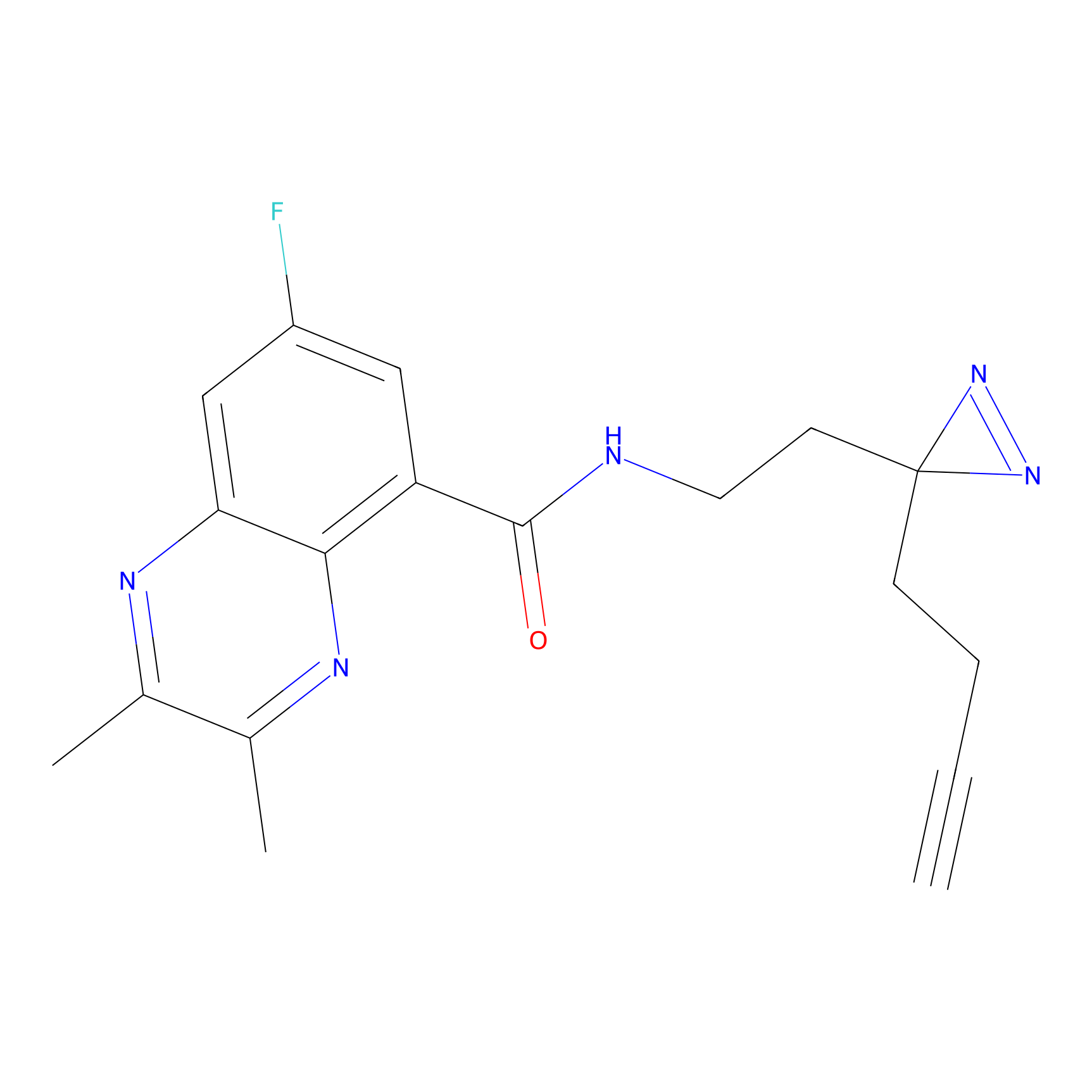
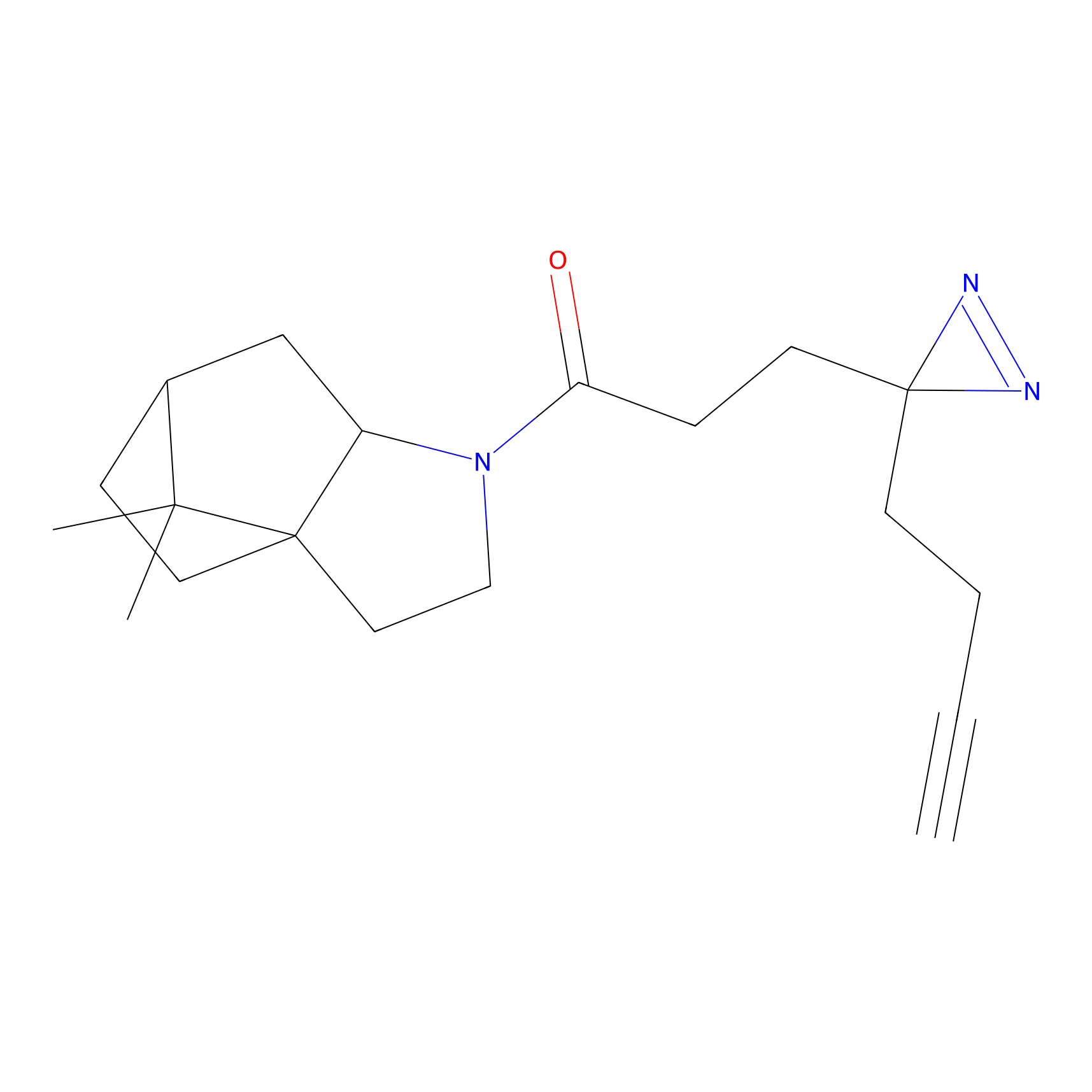
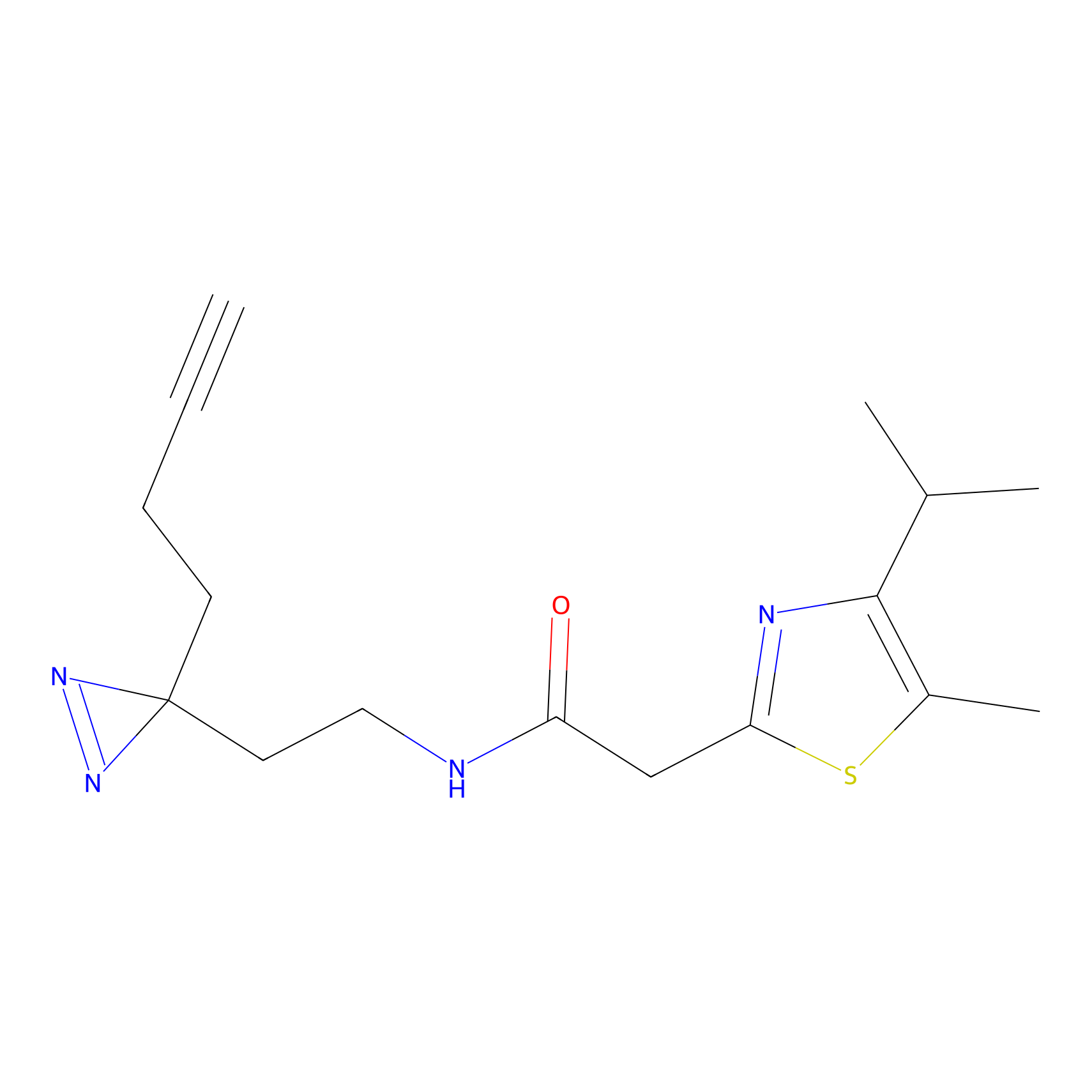
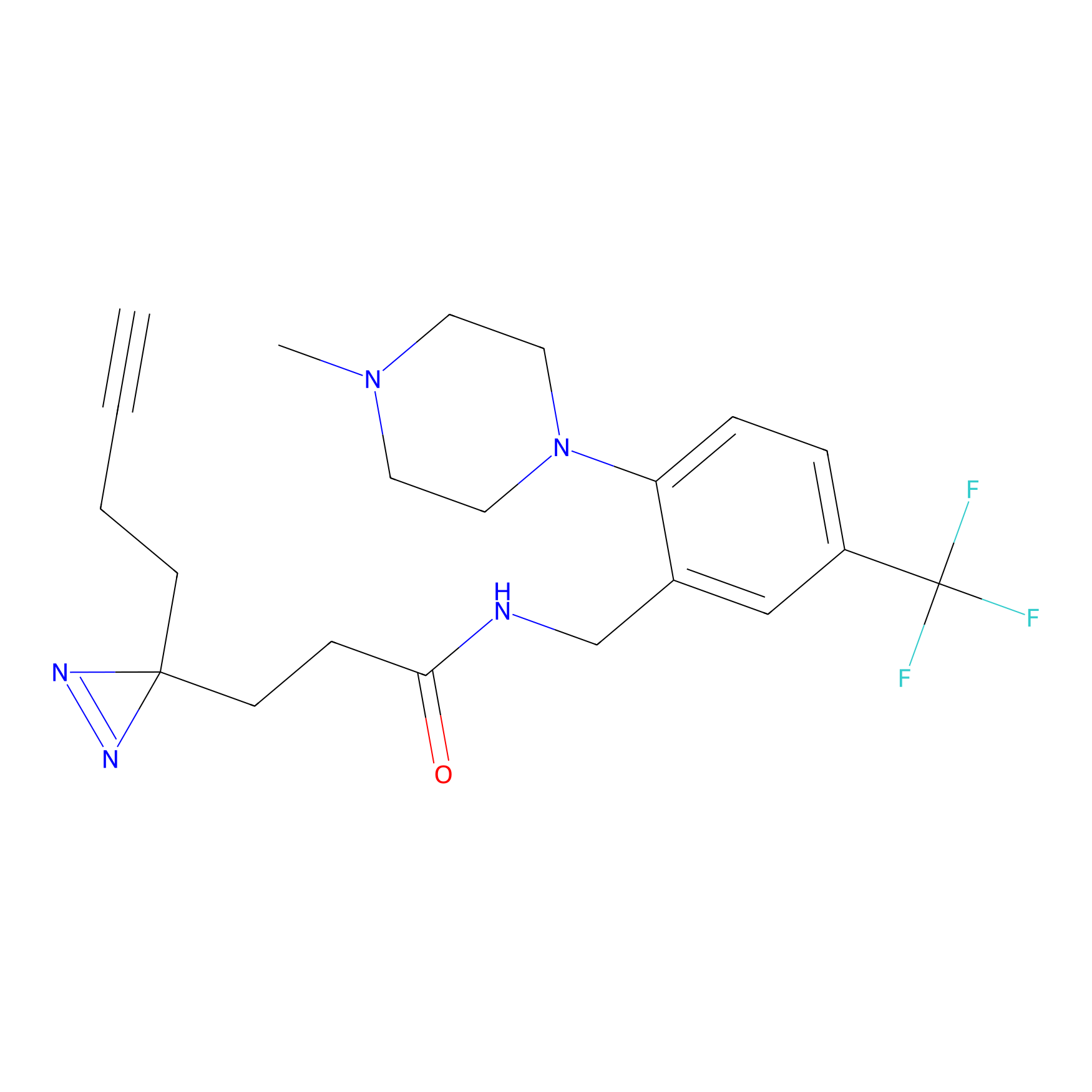
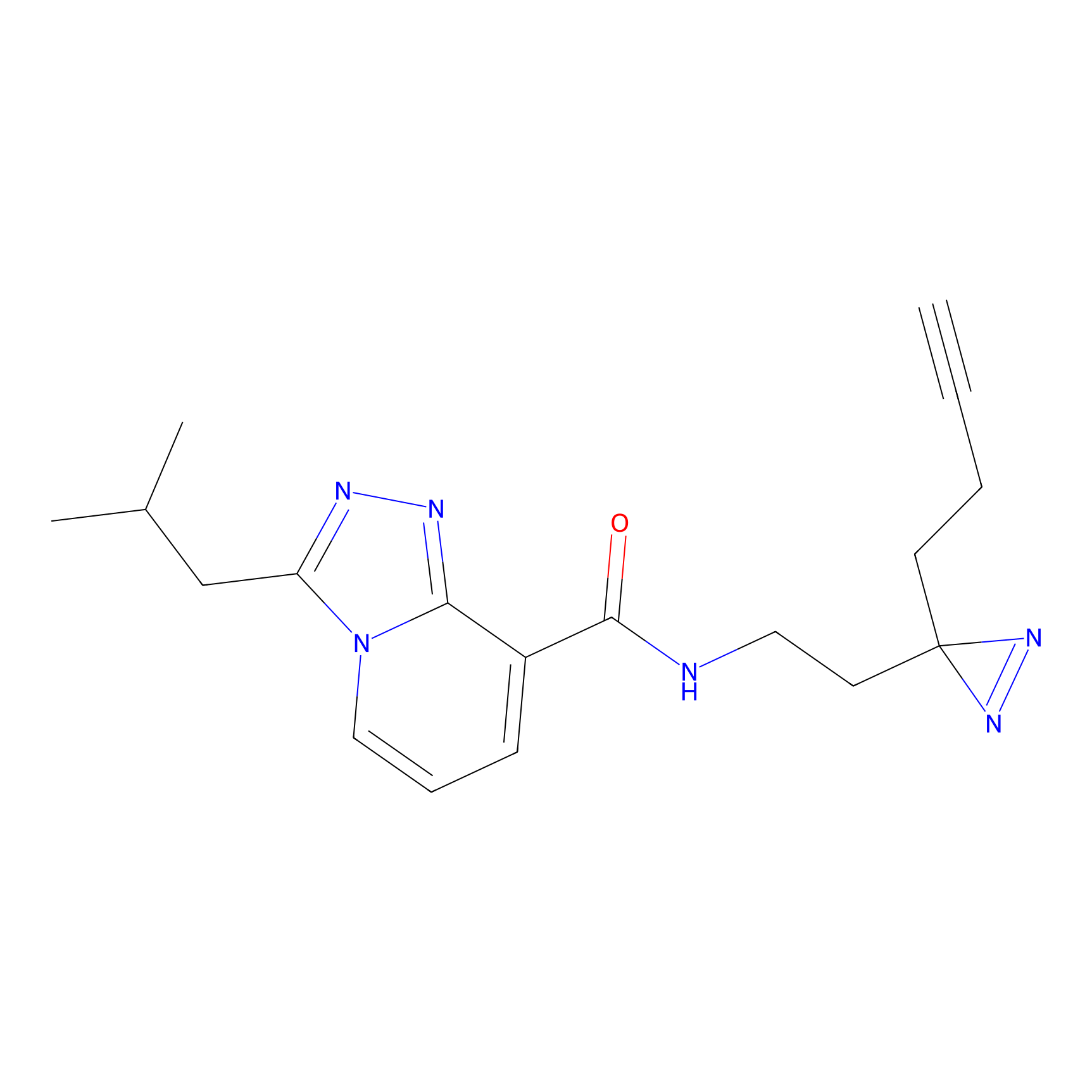
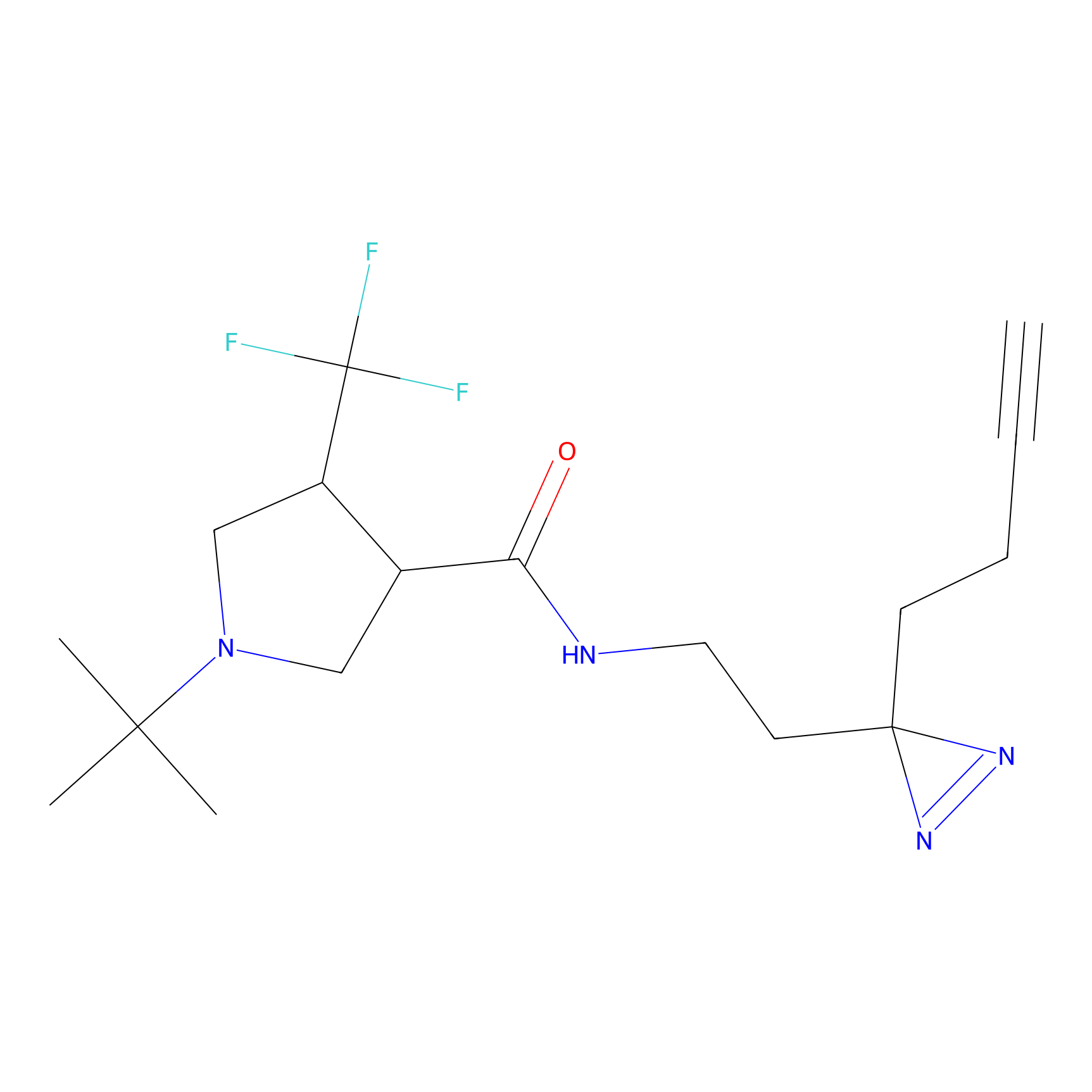
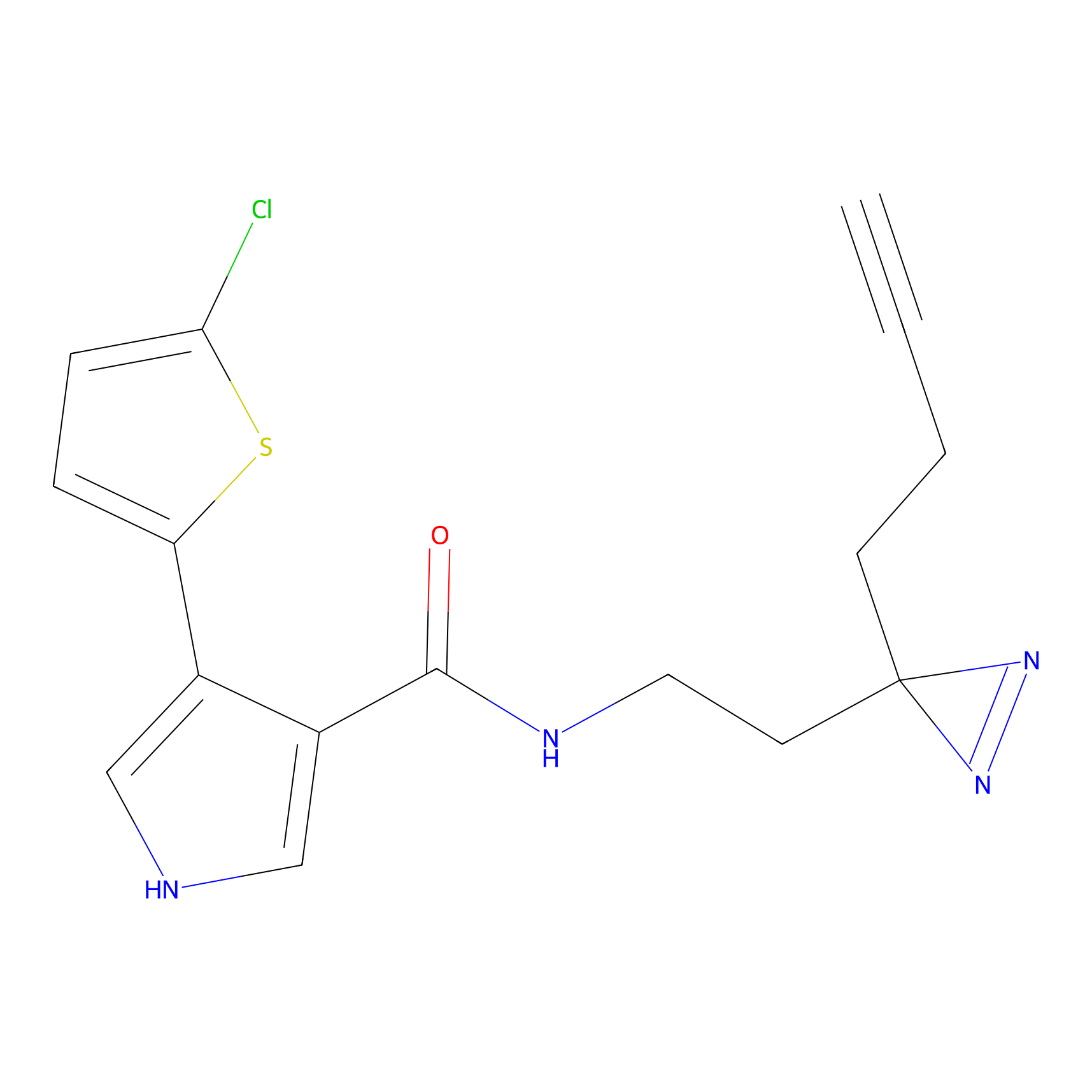
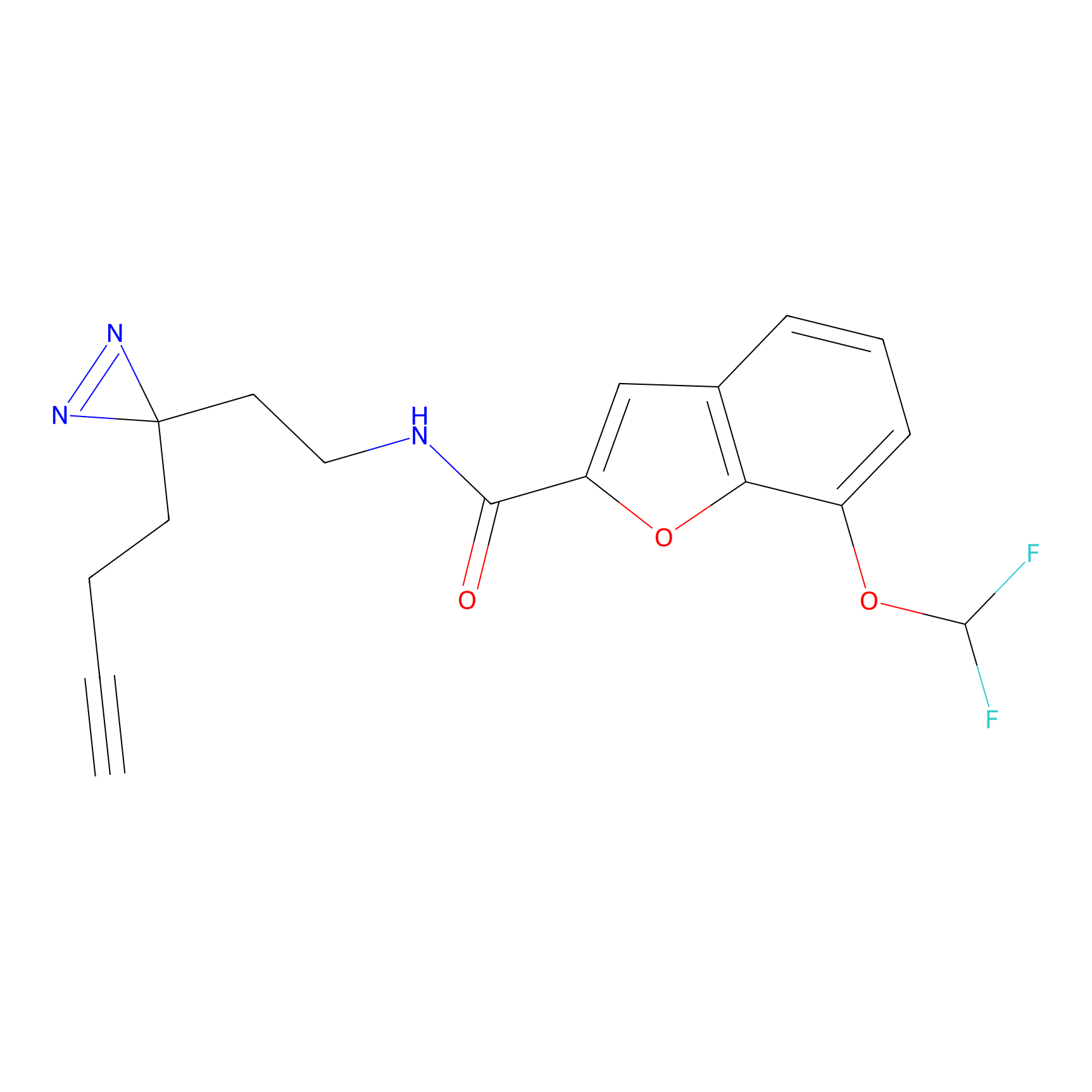
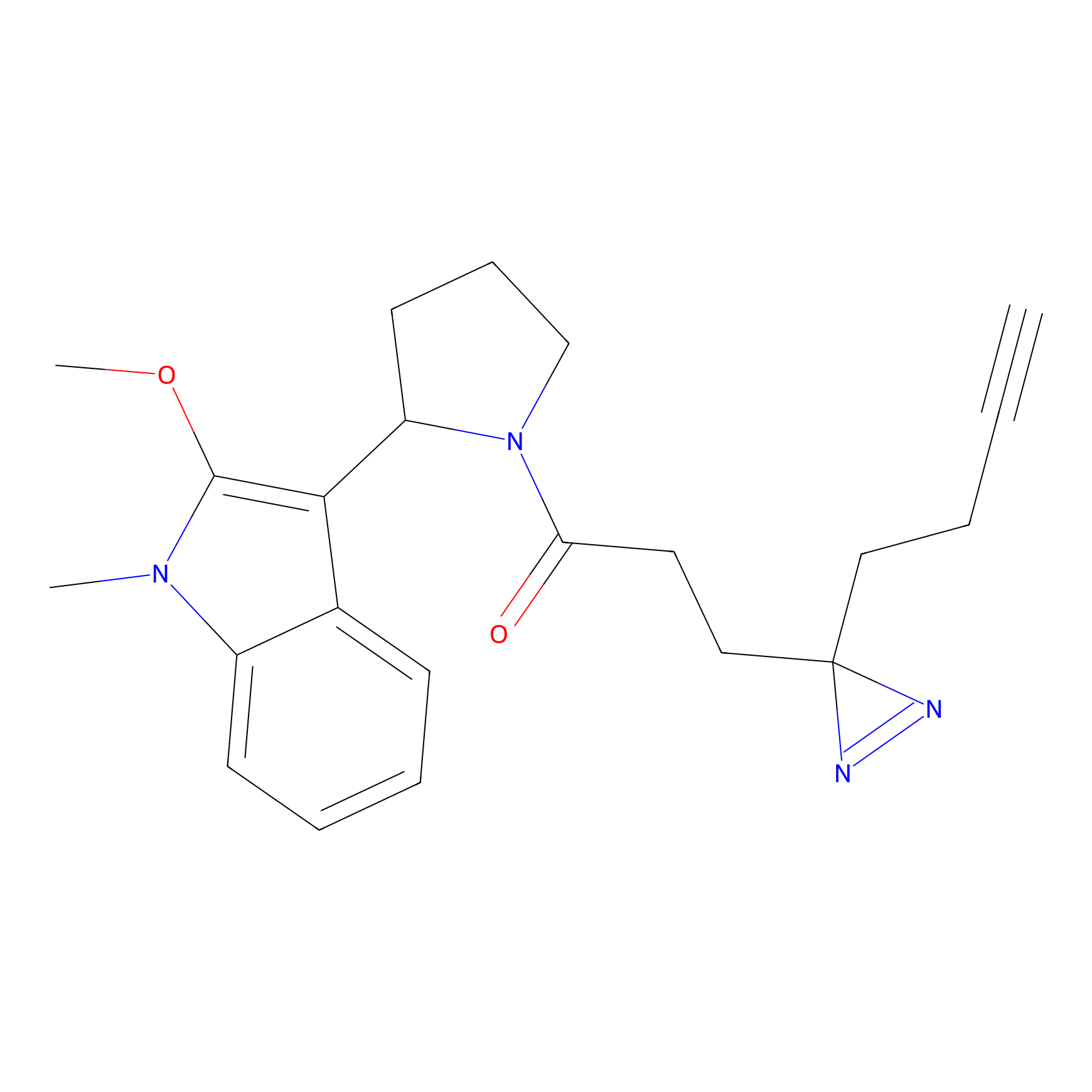
IA-alkyne Probe Info |
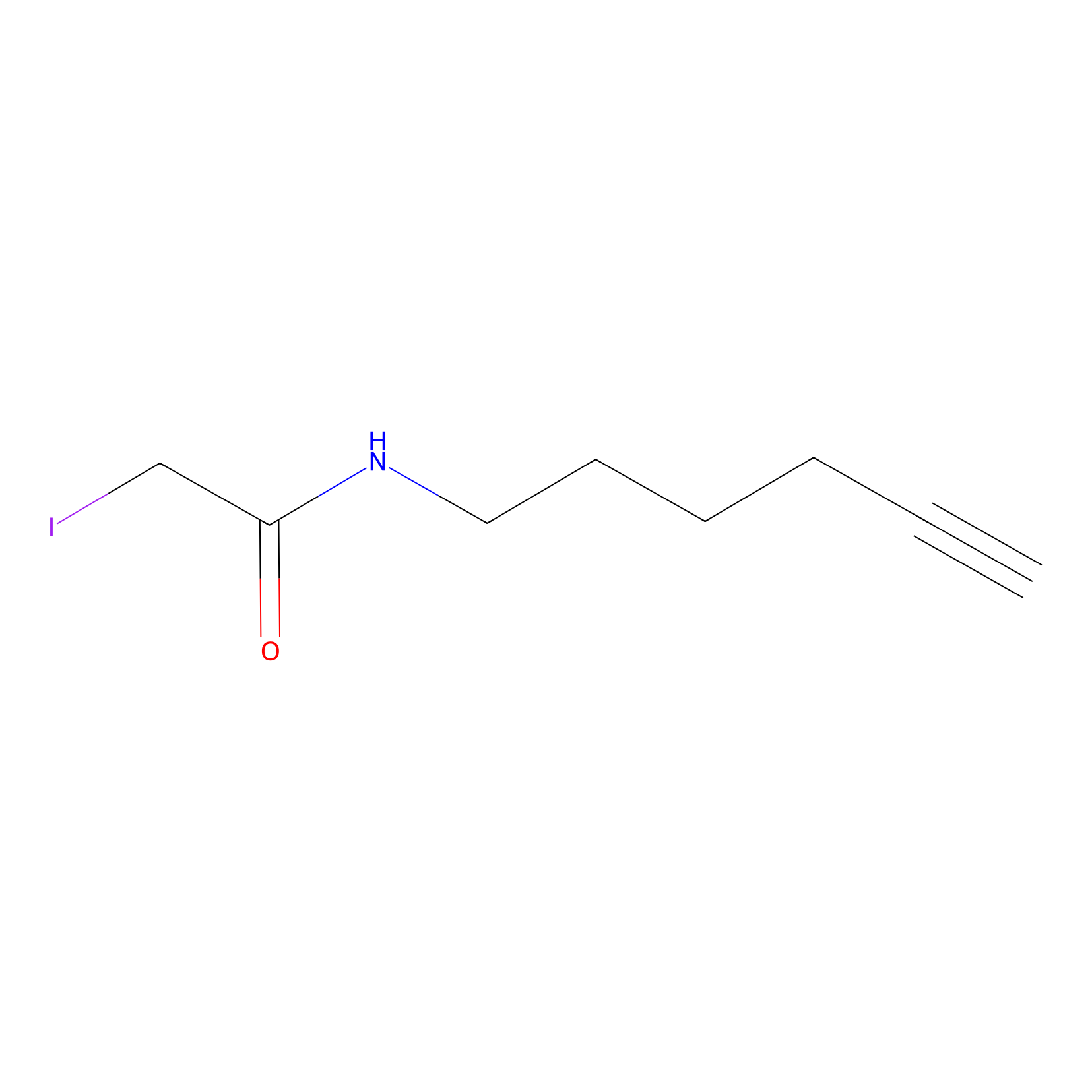 |
N.A. | LDD0165 | [4] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
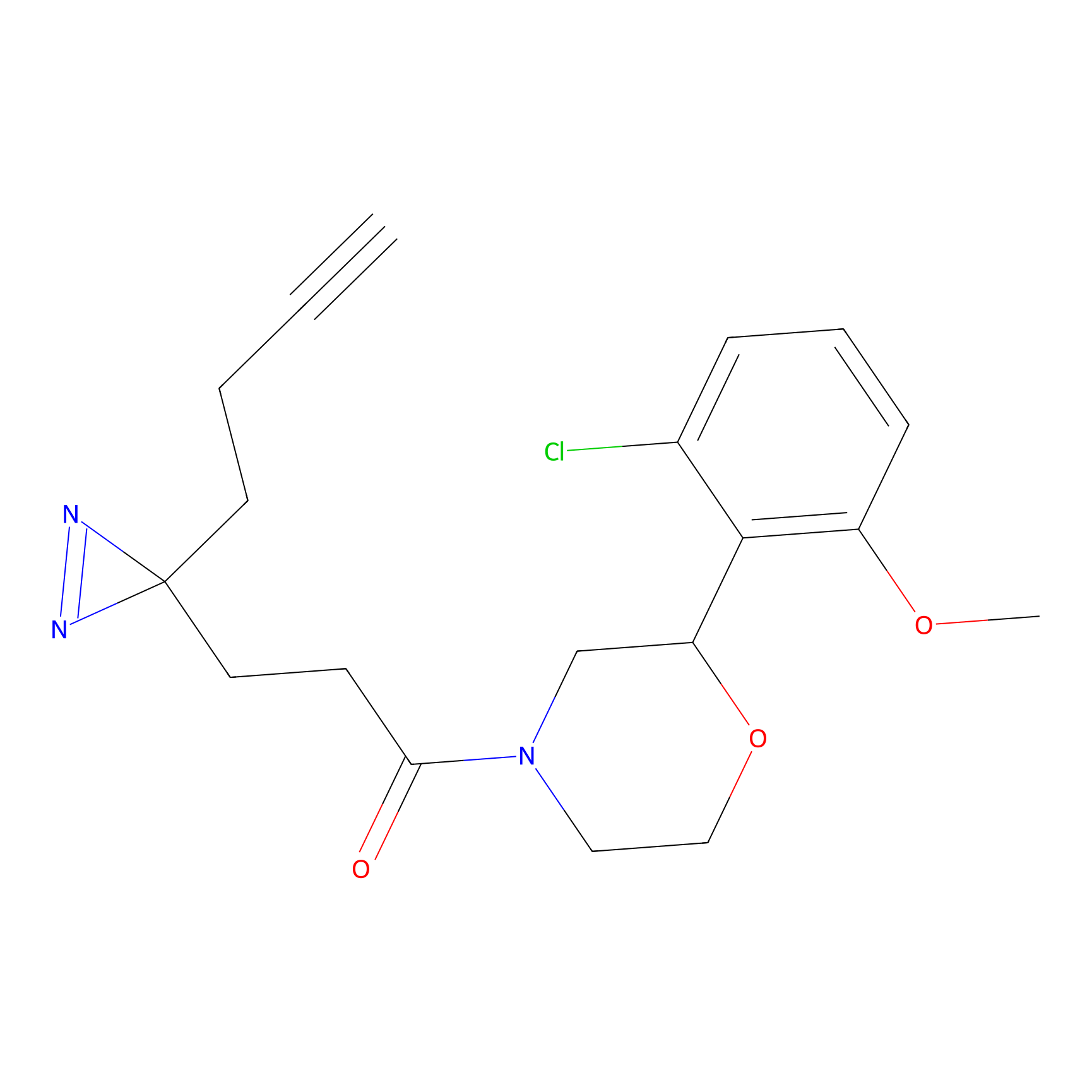
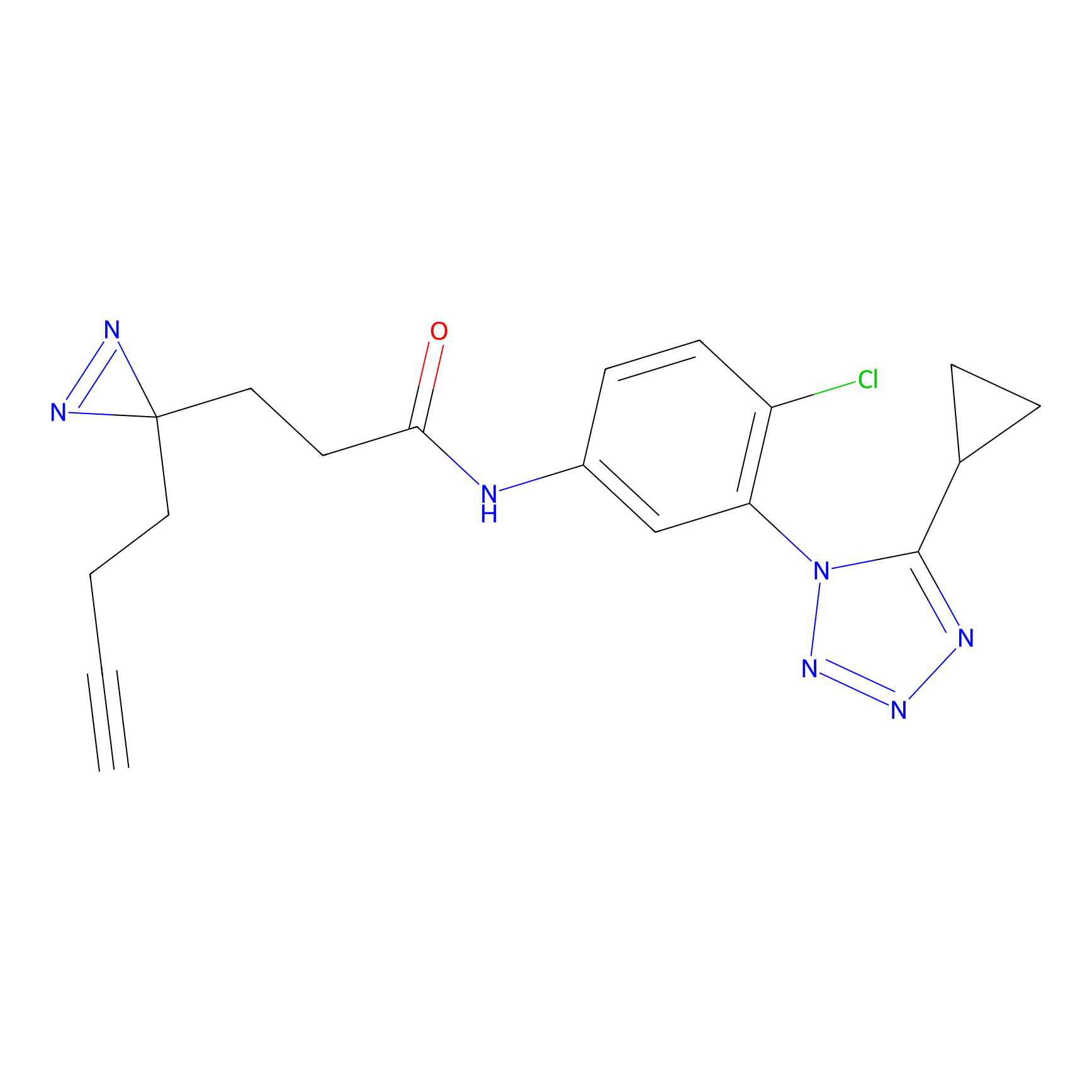
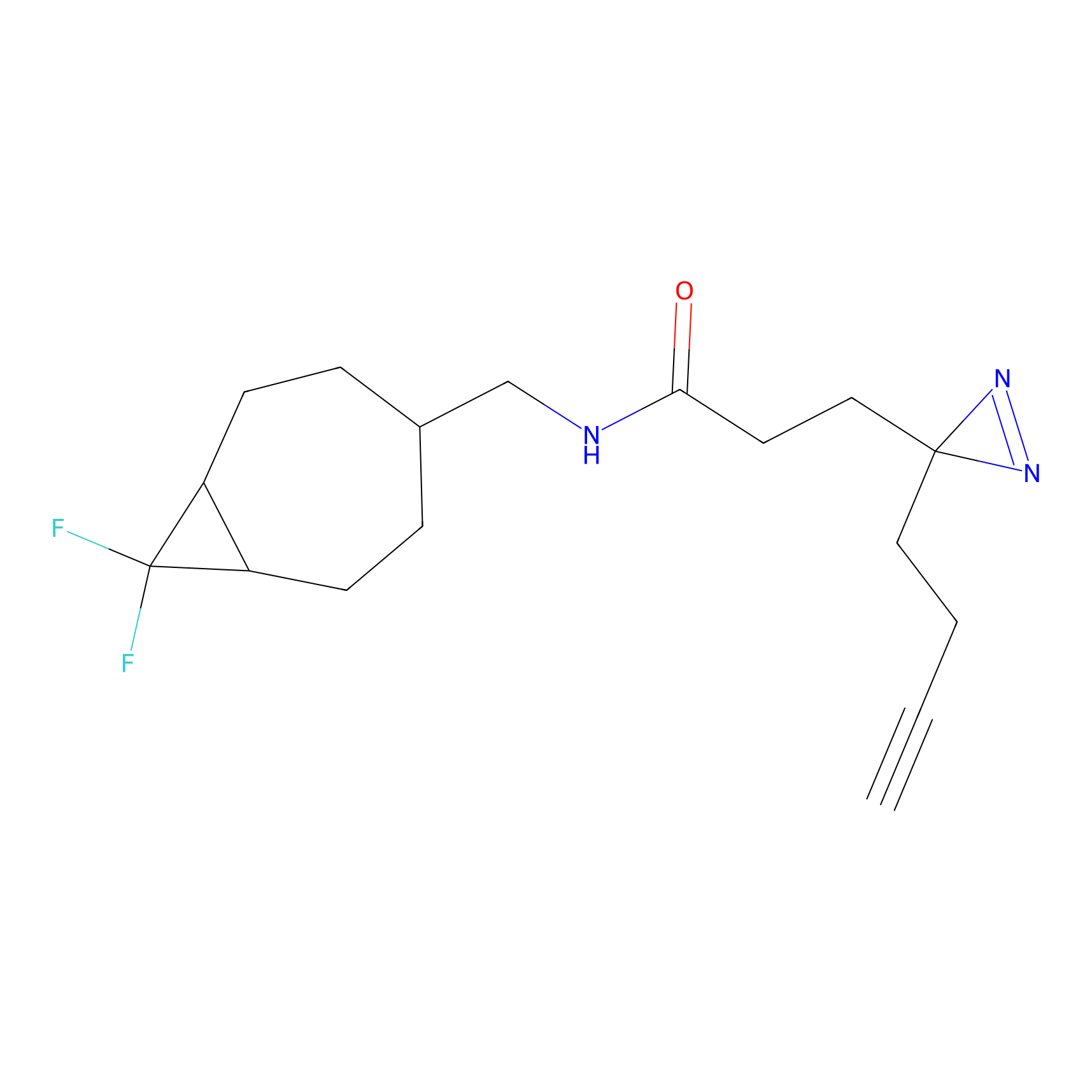
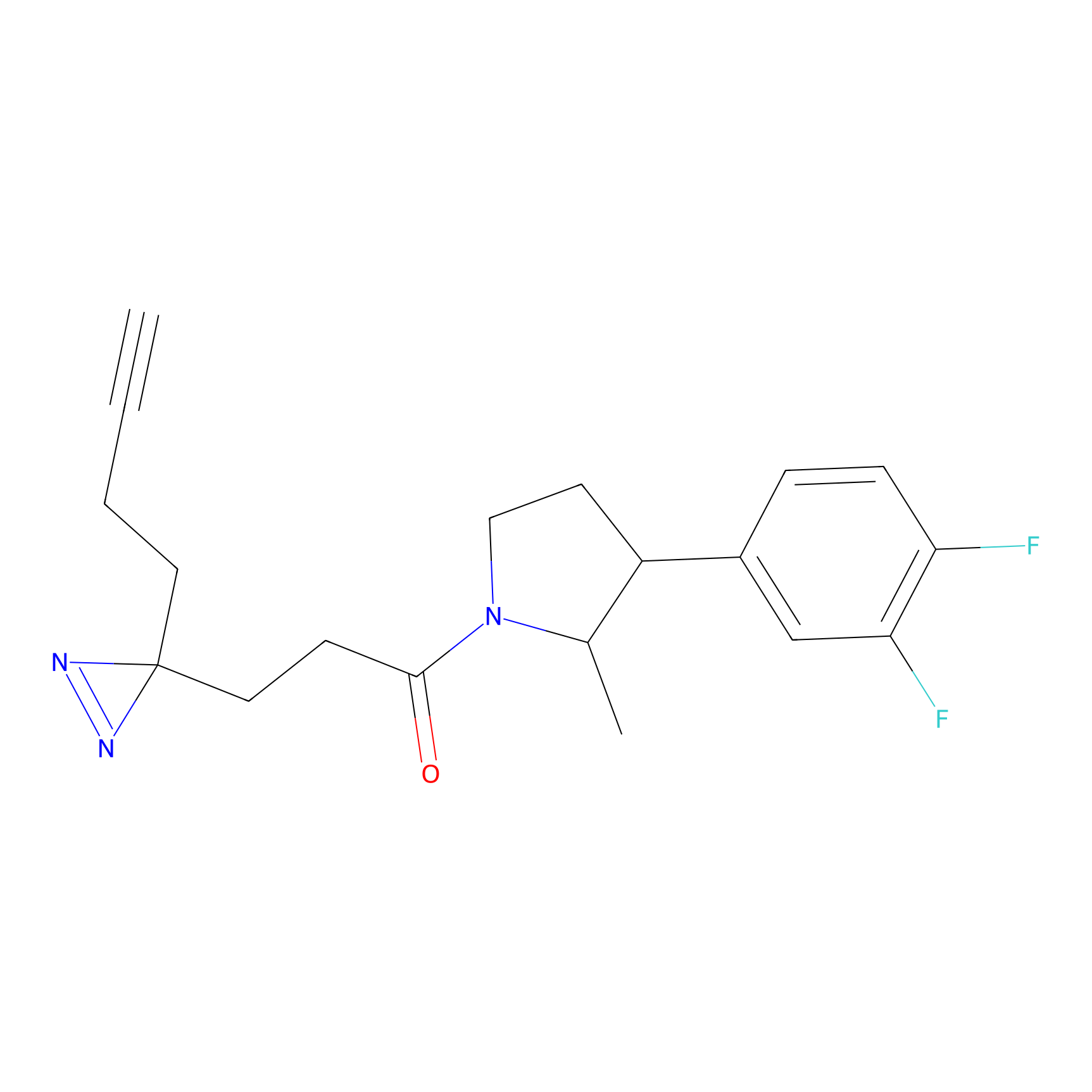
| LDCM0226 | AC11 | HEK-293T | C296(1.14) | LDD1509 | [3] |
| LDCM0270 | AC15 | HEK-293T | C296(1.04) | LDD1513 | [3] |
| LDCM0278 | AC19 | HEK-293T | C296(1.16) | LDD1517 | [3] |
| LDCM0283 | AC23 | HEK-293T | C296(0.92) | LDD1522 | [3] |
| LDCM0287 | AC27 | HEK-293T | C296(0.91) | LDD1526 | [3] |
| LDCM0290 | AC3 | HEK-293T | C296(0.86) | LDD1529 | [3] |
| LDCM0292 | AC31 | HEK-293T | C296(0.91) | LDD1531 | [3] |
| LDCM0296 | AC35 | HEK-293T | C296(1.11) | LDD1535 | [3] |
| LDCM0300 | AC39 | HEK-293T | C296(1.02) | LDD1539 | [3] |
| LDCM0305 | AC43 | HEK-293T | C296(1.06) | LDD1544 | [3] |
| LDCM0309 | AC47 | HEK-293T | C296(1.00) | LDD1548 | [3] |
| LDCM0314 | AC51 | HEK-293T | C296(1.11) | LDD1553 | [3] |
| LDCM0318 | AC55 | HEK-293T | C296(0.86) | LDD1557 | [3] |
| LDCM0322 | AC59 | HEK-293T | C296(0.91) | LDD1561 | [3] |
| LDCM0327 | AC63 | HEK-293T | C296(0.98) | LDD1566 | [3] |
| LDCM0334 | AC7 | HEK-293T | C296(0.96) | LDD1568 | [3] |
| LDCM0379 | CL11 | HEK-293T | C296(0.92) | LDD1583 | [3] |
| LDCM0406 | CL19 | HEK-293T | C296(1.25) | LDD1610 | [3] |
| LDCM0411 | CL23 | HEK-293T | C296(0.97) | LDD1615 | [3] |
| LDCM0420 | CL31 | HEK-293T | C296(1.02) | LDD1624 | [3] |
| LDCM0424 | CL35 | HEK-293T | C296(1.06) | LDD1628 | [3] |
| LDCM0433 | CL43 | HEK-293T | C296(1.05) | LDD1637 | [3] |
| LDCM0437 | CL47 | HEK-293T | C296(0.99) | LDD1641 | [3] |
| LDCM0446 | CL55 | HEK-293T | C296(1.00) | LDD1649 | [3] |
| LDCM0450 | CL59 | HEK-293T | C296(0.91) | LDD1653 | [3] |
| LDCM0459 | CL67 | HEK-293T | C296(0.93) | LDD1662 | [3] |
| LDCM0462 | CL7 | HEK-293T | C296(1.03) | LDD1665 | [3] |
| LDCM0464 | CL71 | HEK-293T | C296(1.05) | LDD1667 | [3] |
| LDCM0472 | CL79 | HEK-293T | C296(0.86) | LDD1675 | [3] |
| LDCM0477 | CL83 | HEK-293T | C296(1.21) | LDD1680 | [3] |
| LDCM0486 | CL91 | HEK-293T | C296(0.80) | LDD1689 | [3] |
| LDCM0490 | CL95 | HEK-293T | C296(0.95) | LDD1693 | [3] |
References