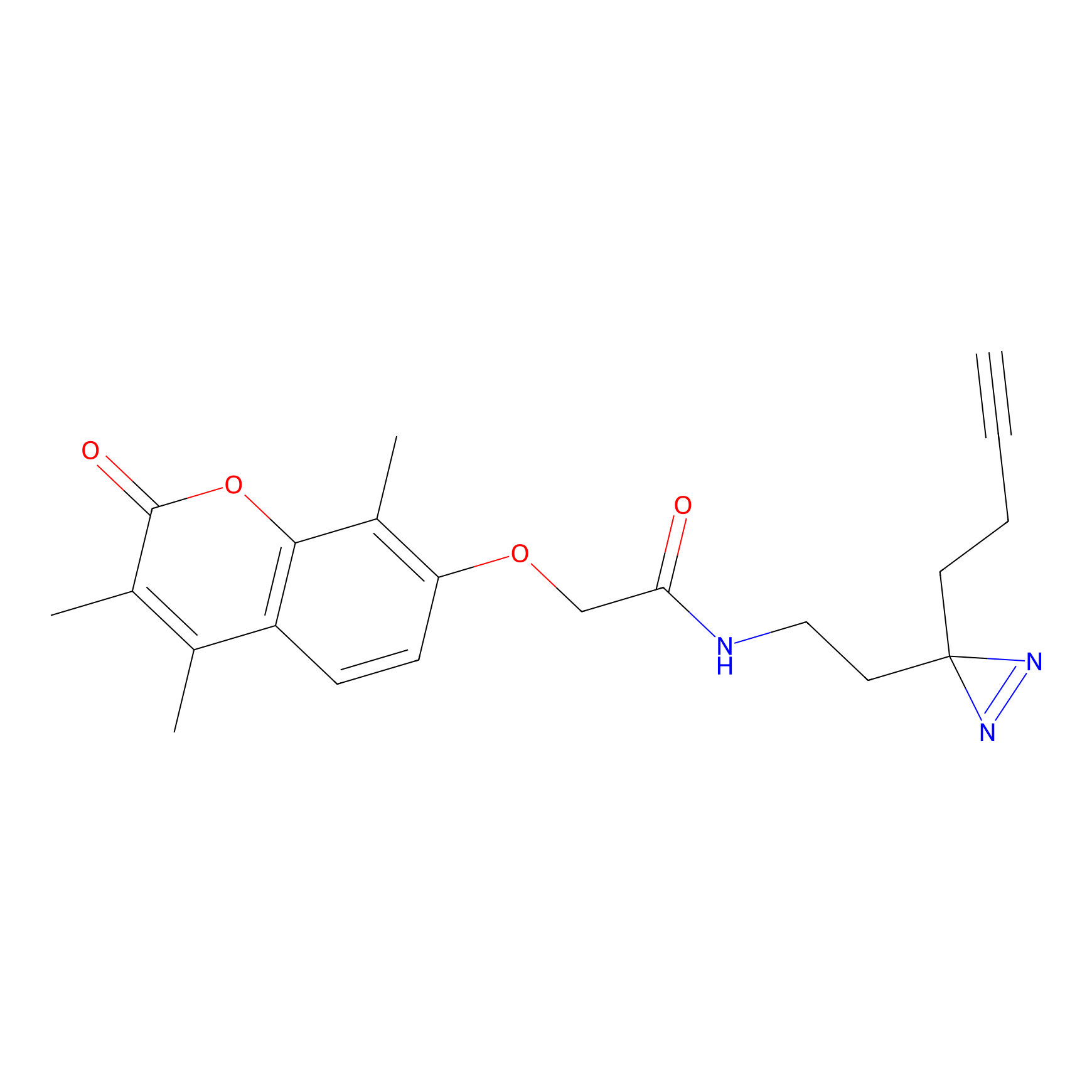
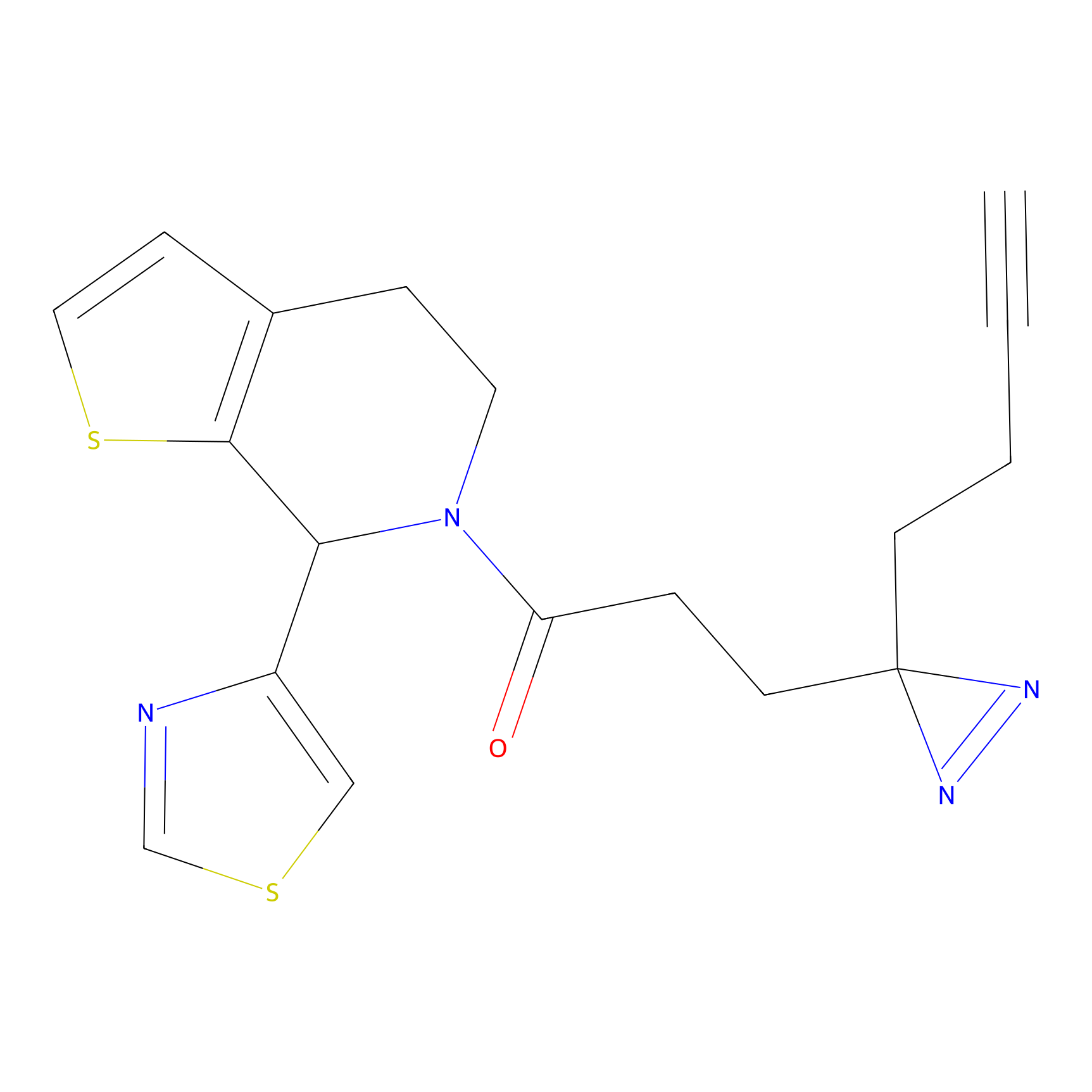
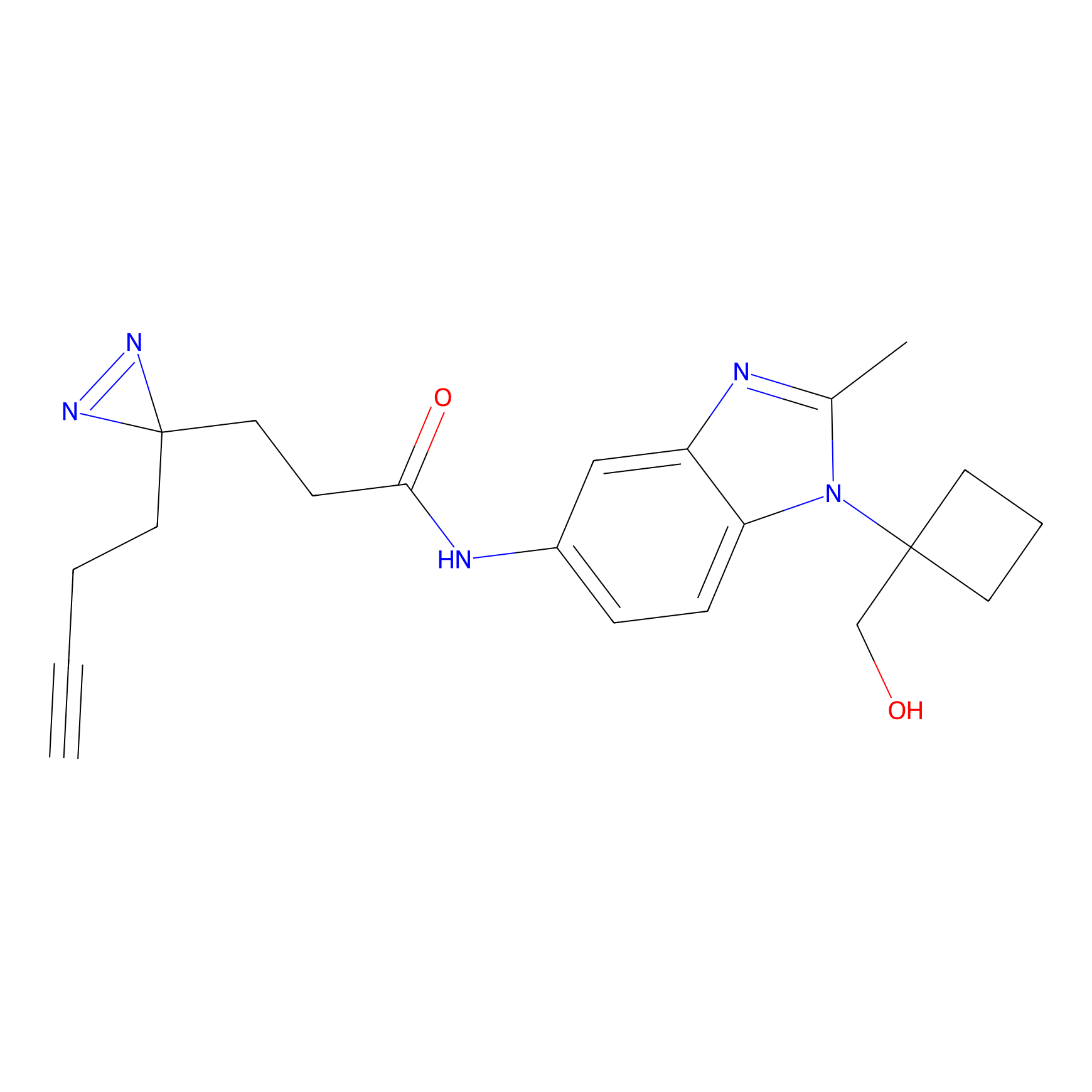
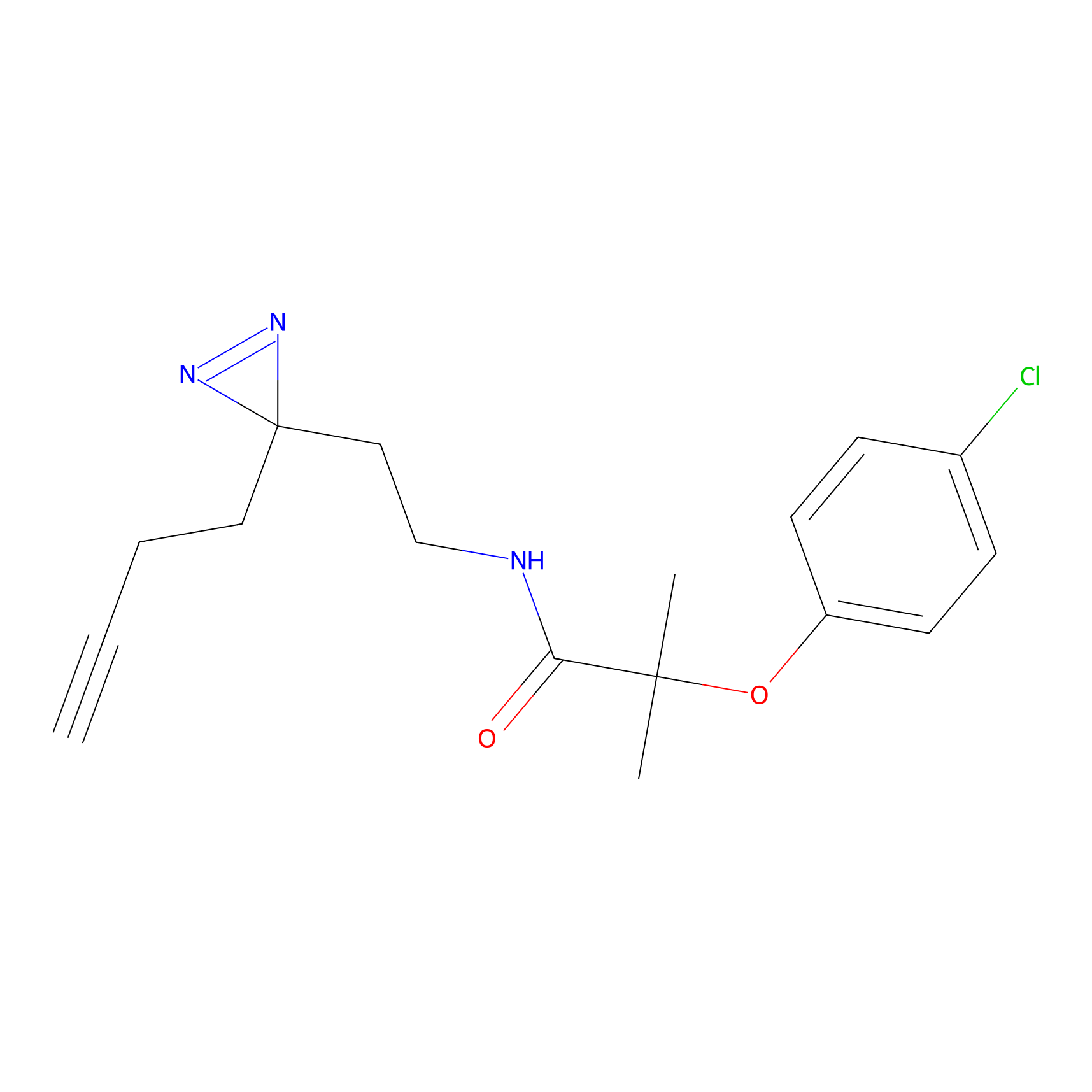
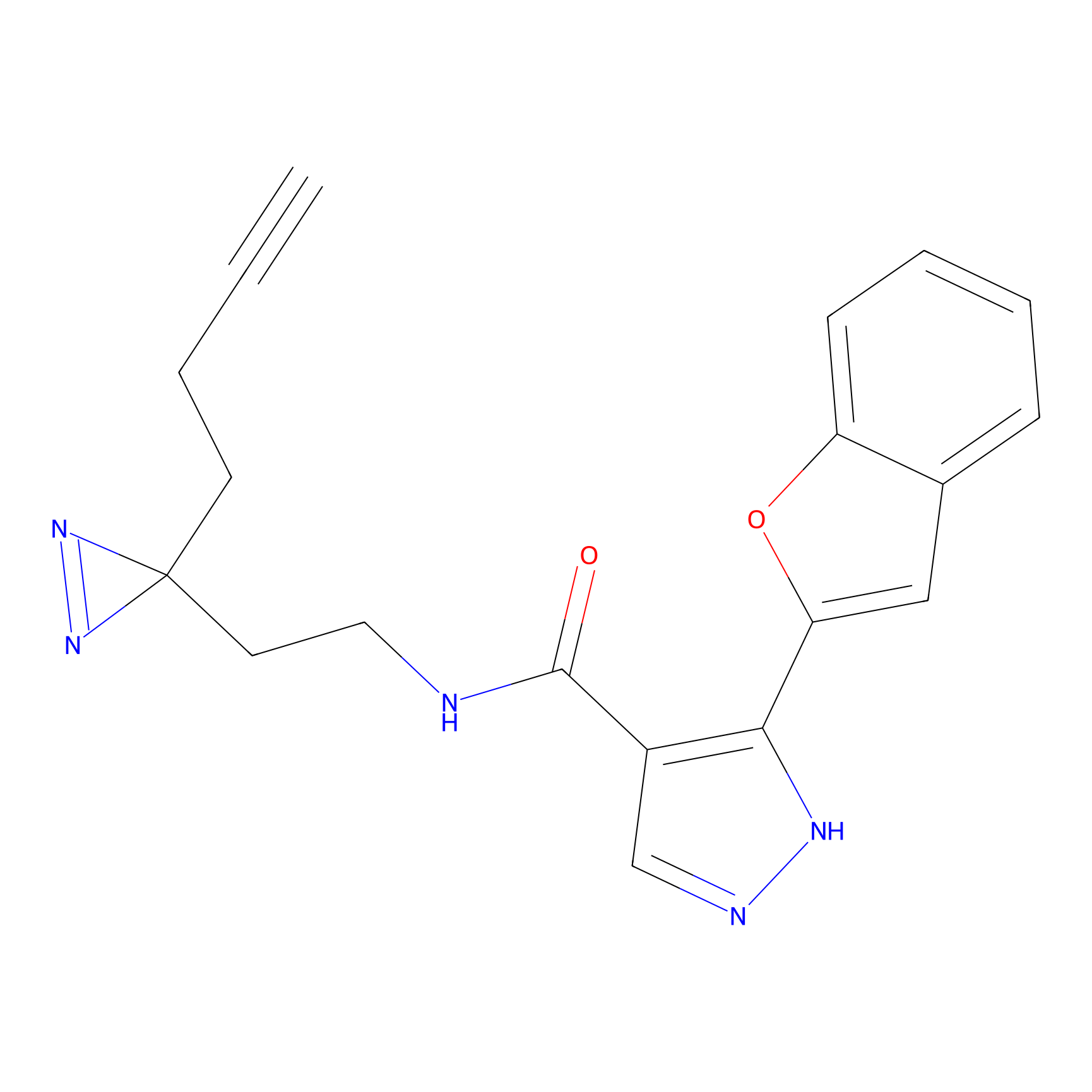
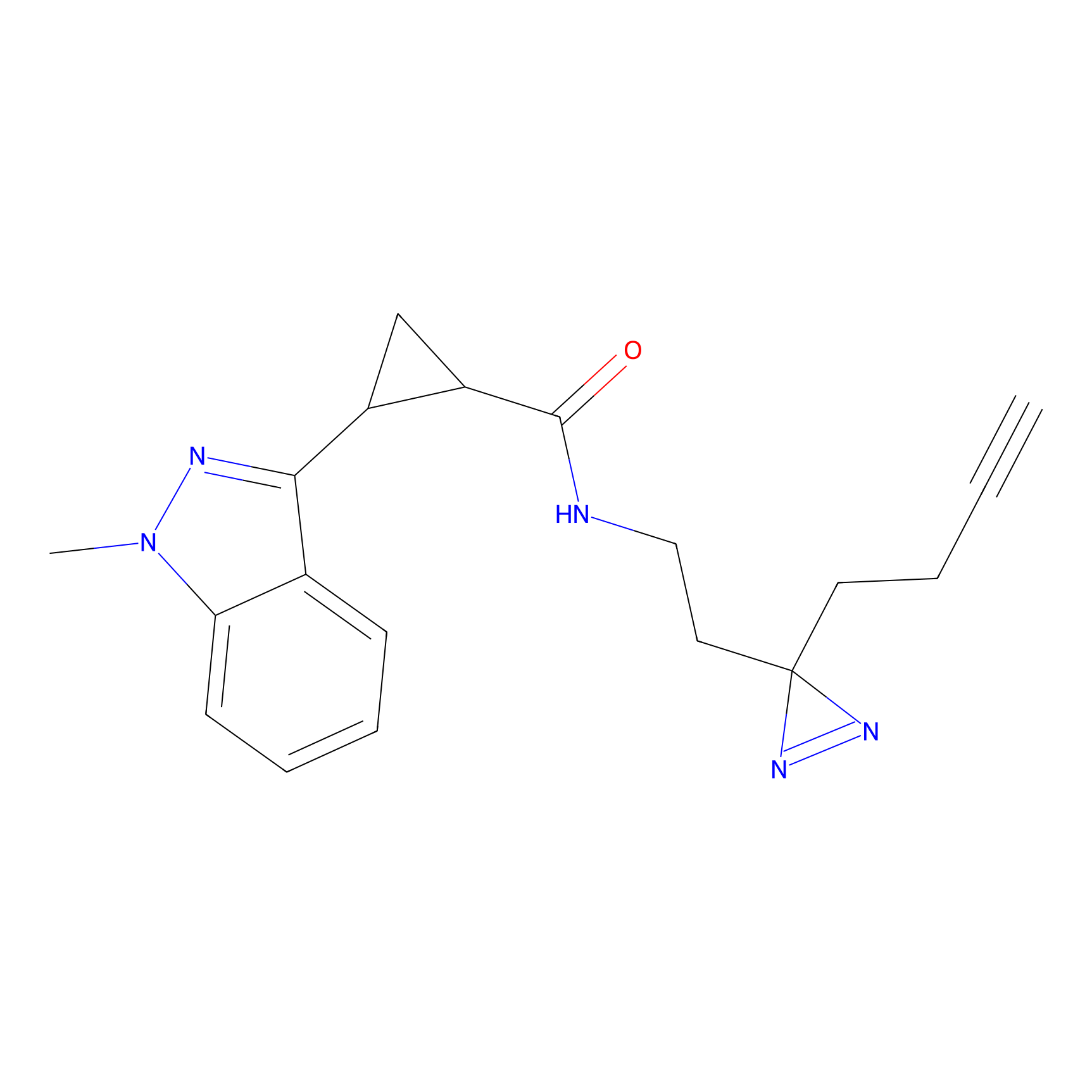
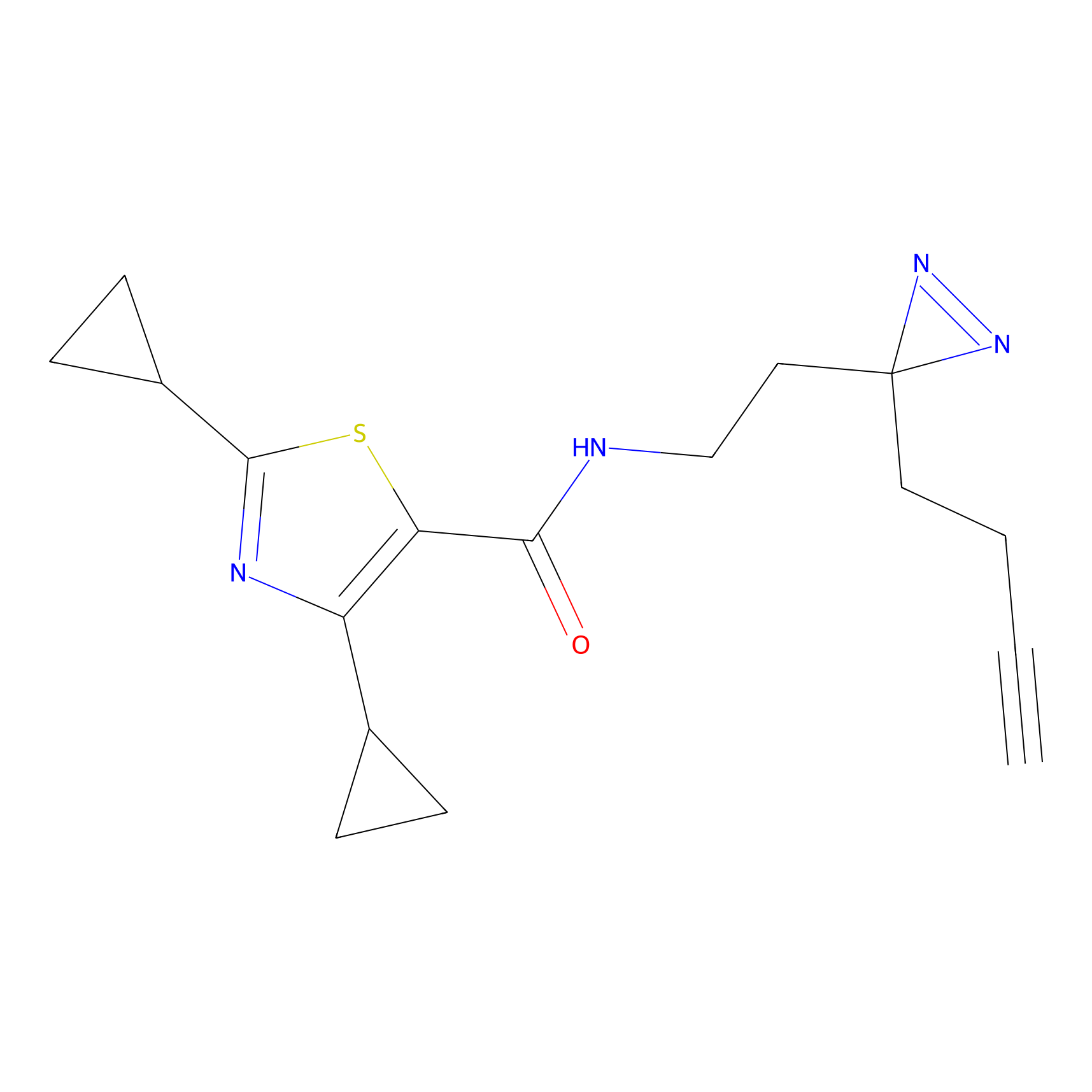
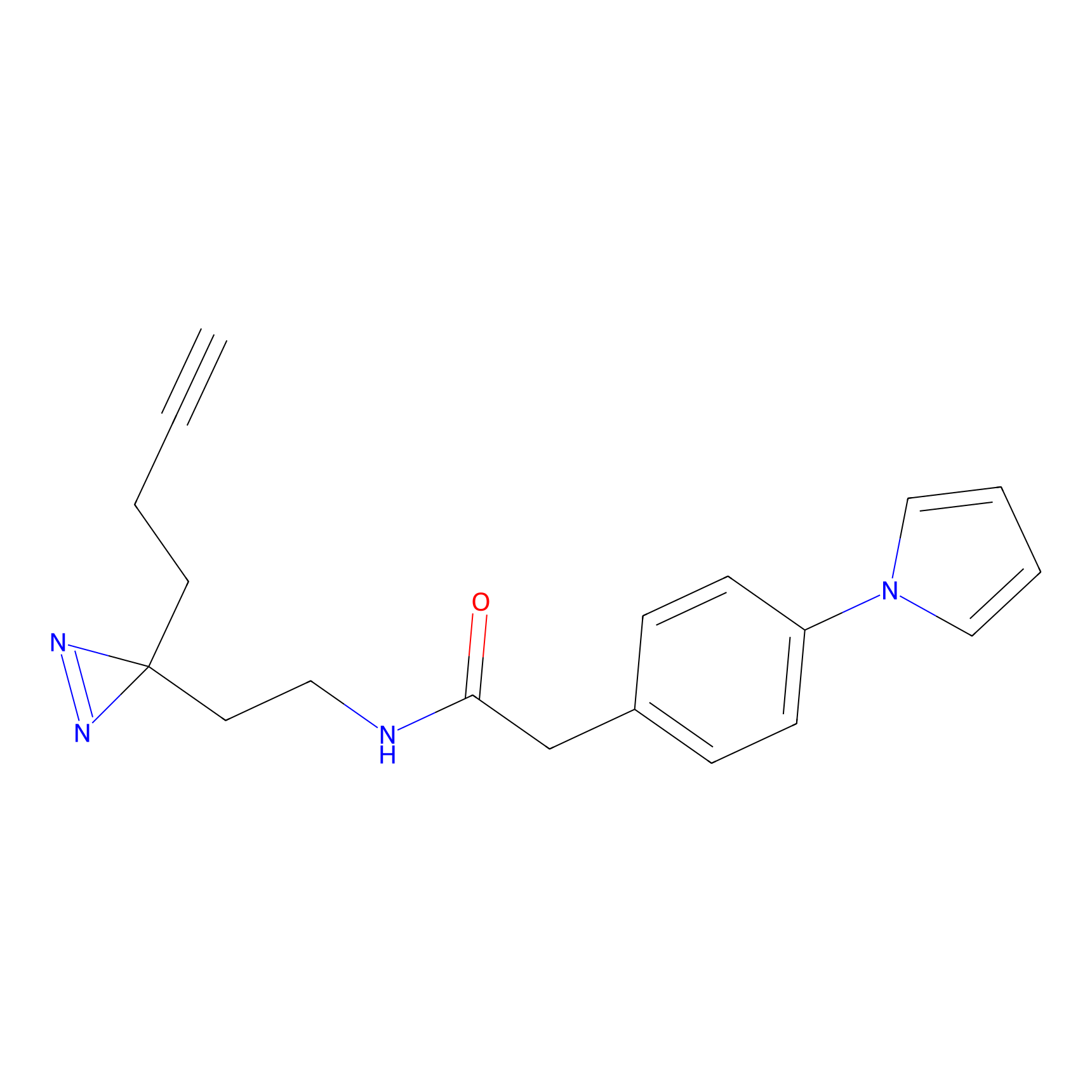
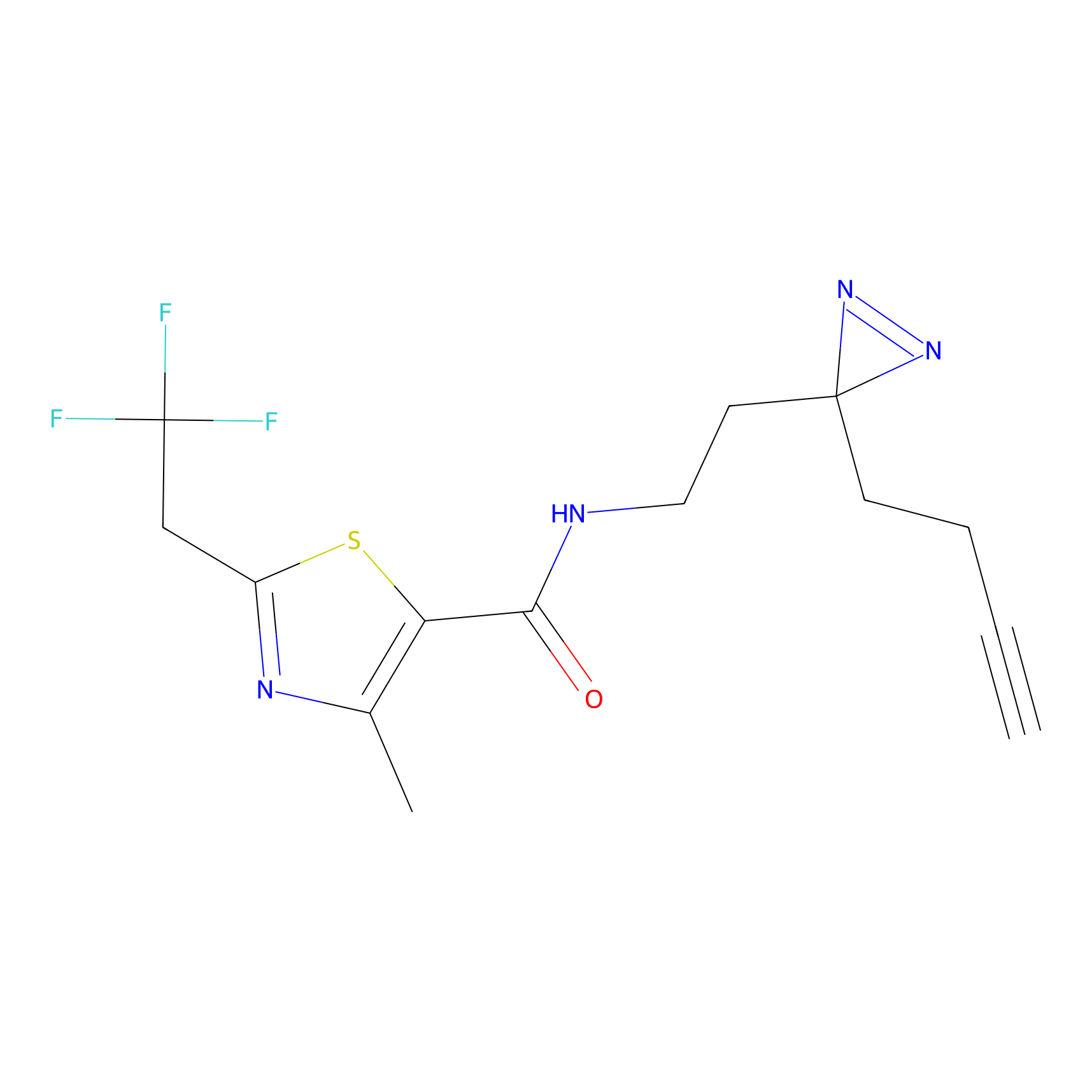
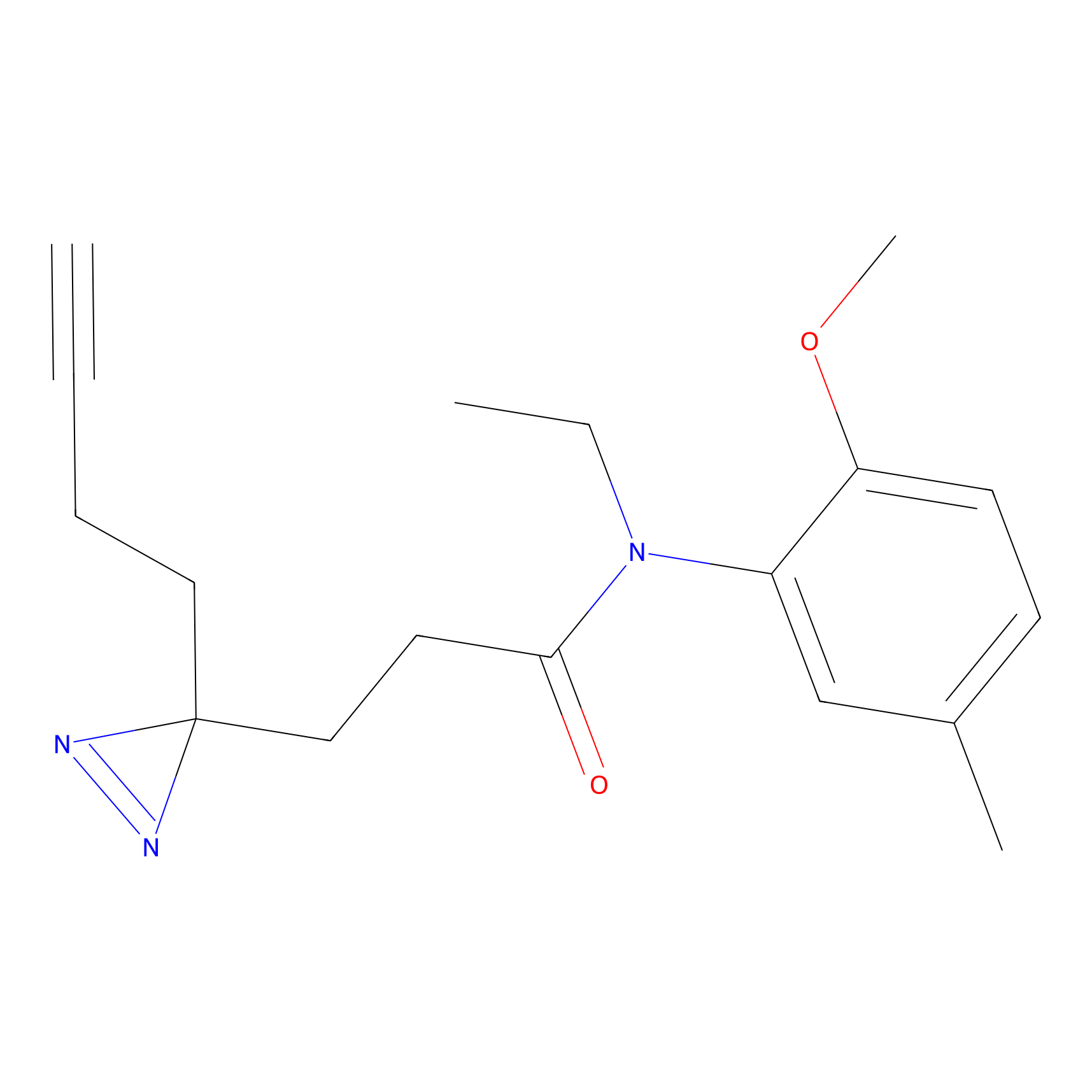
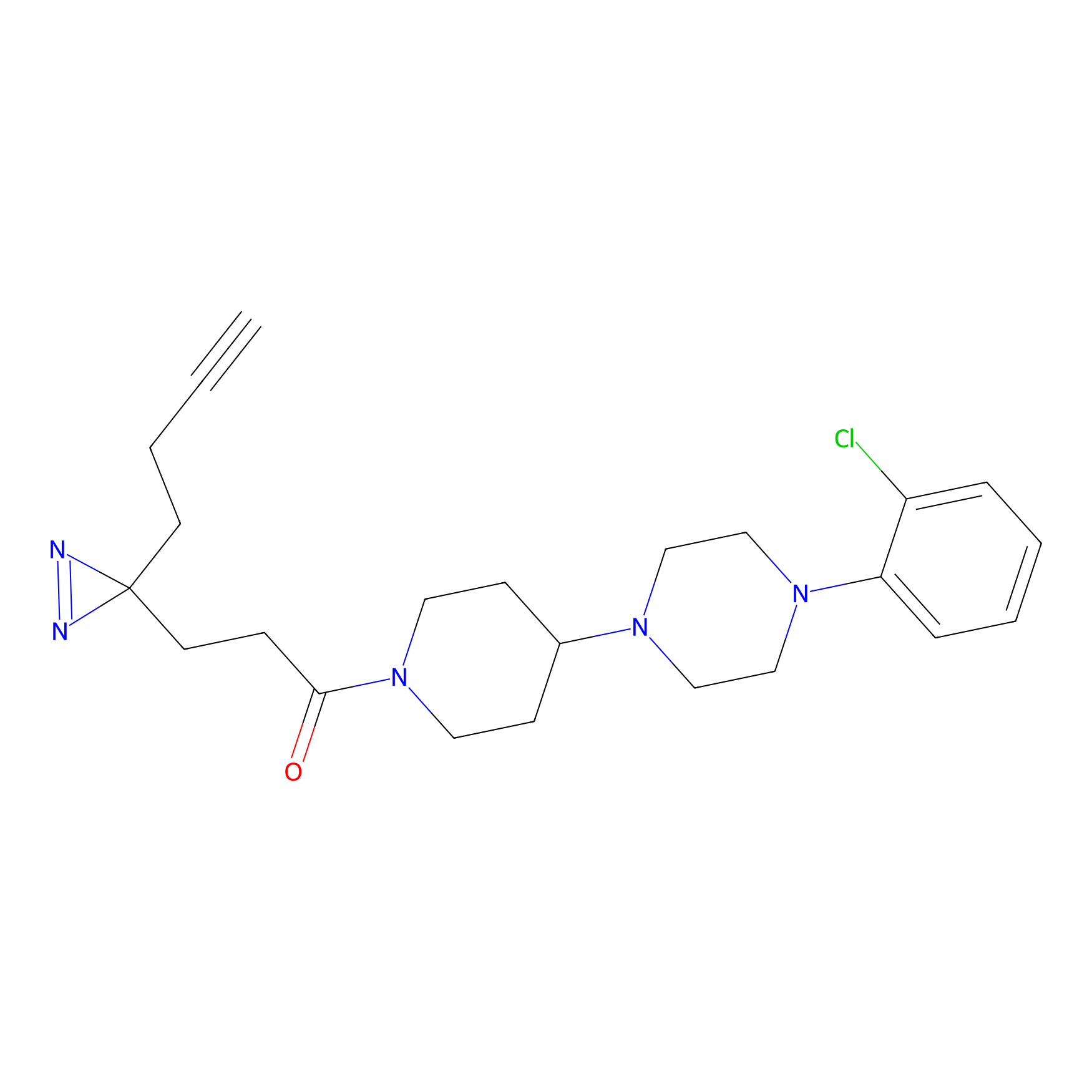
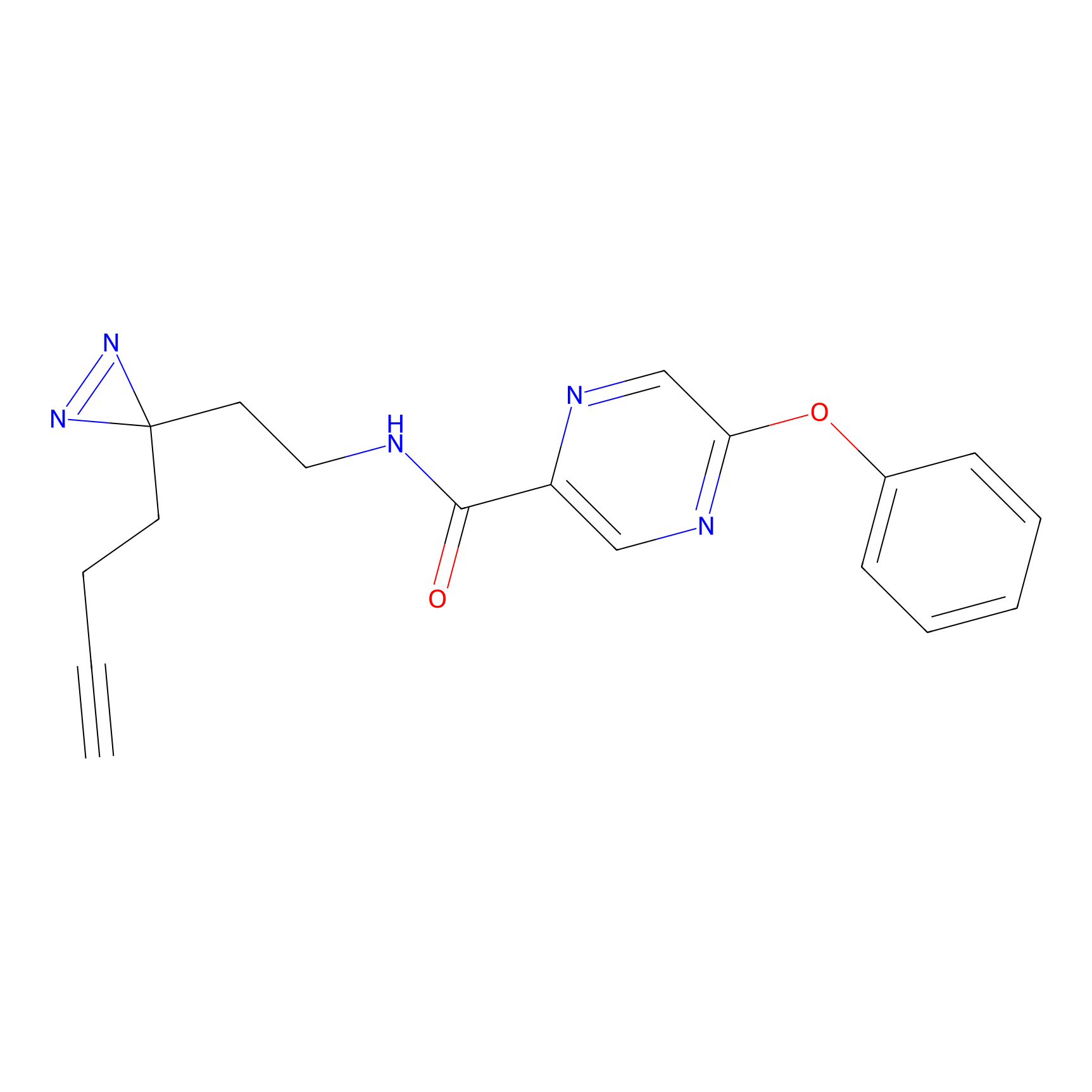
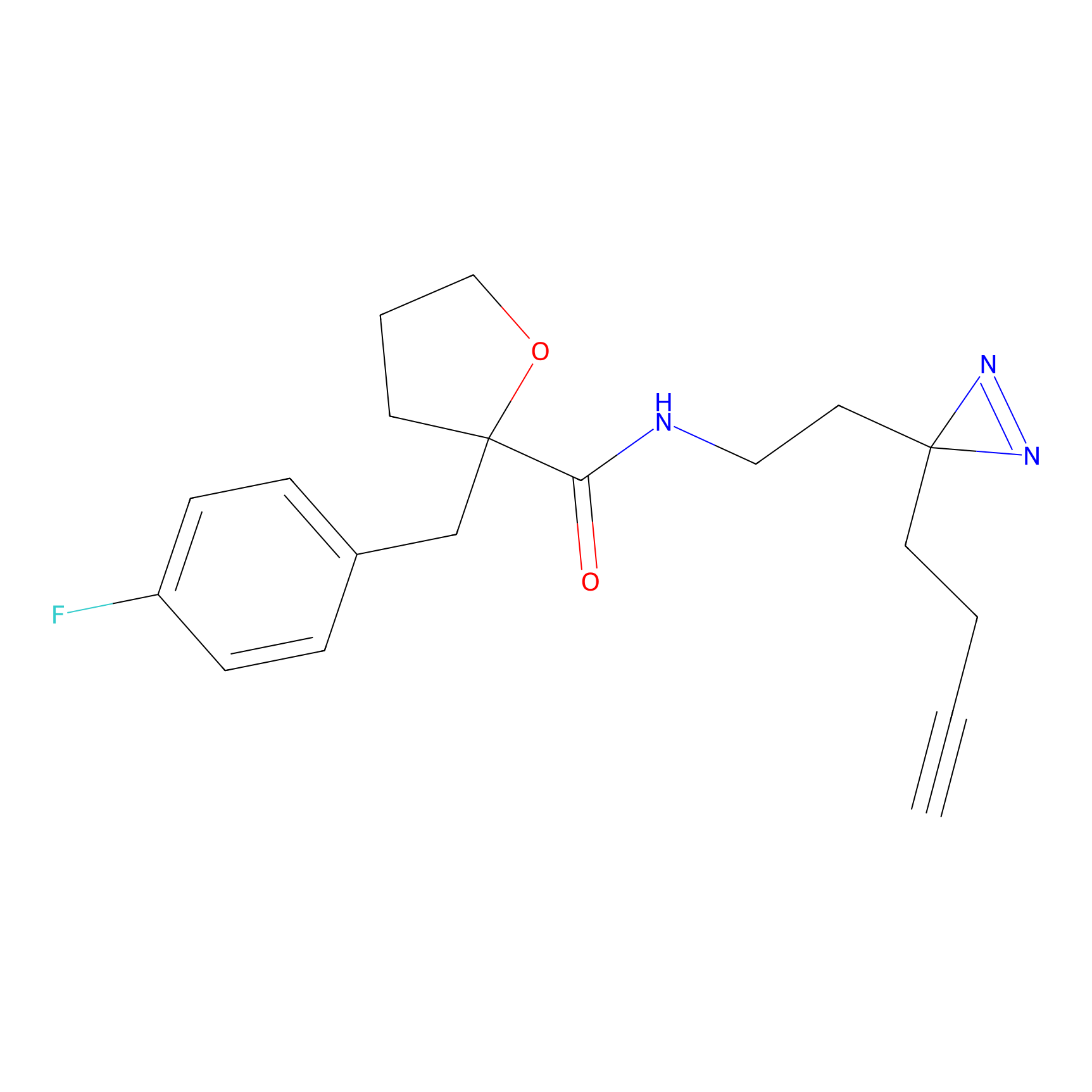
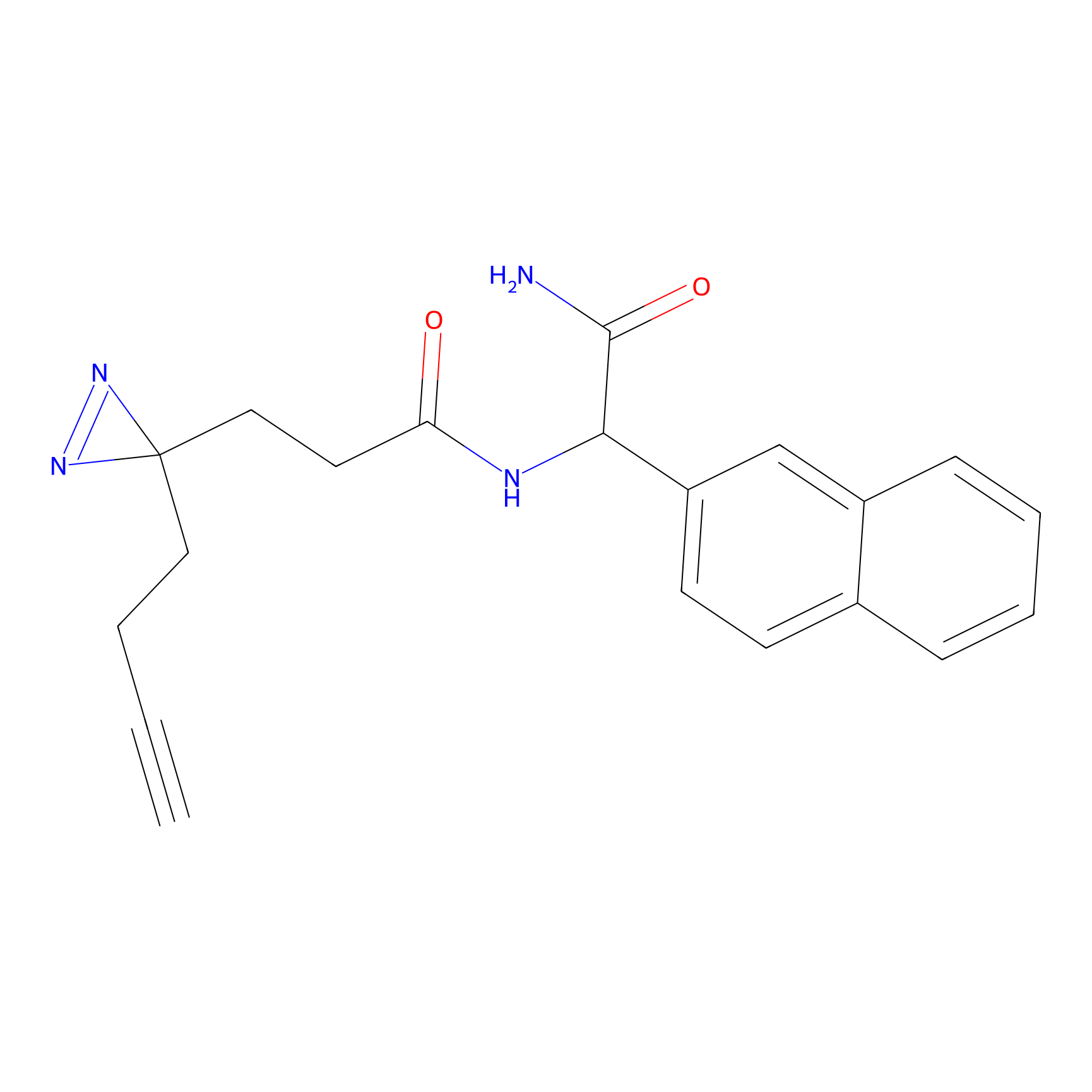
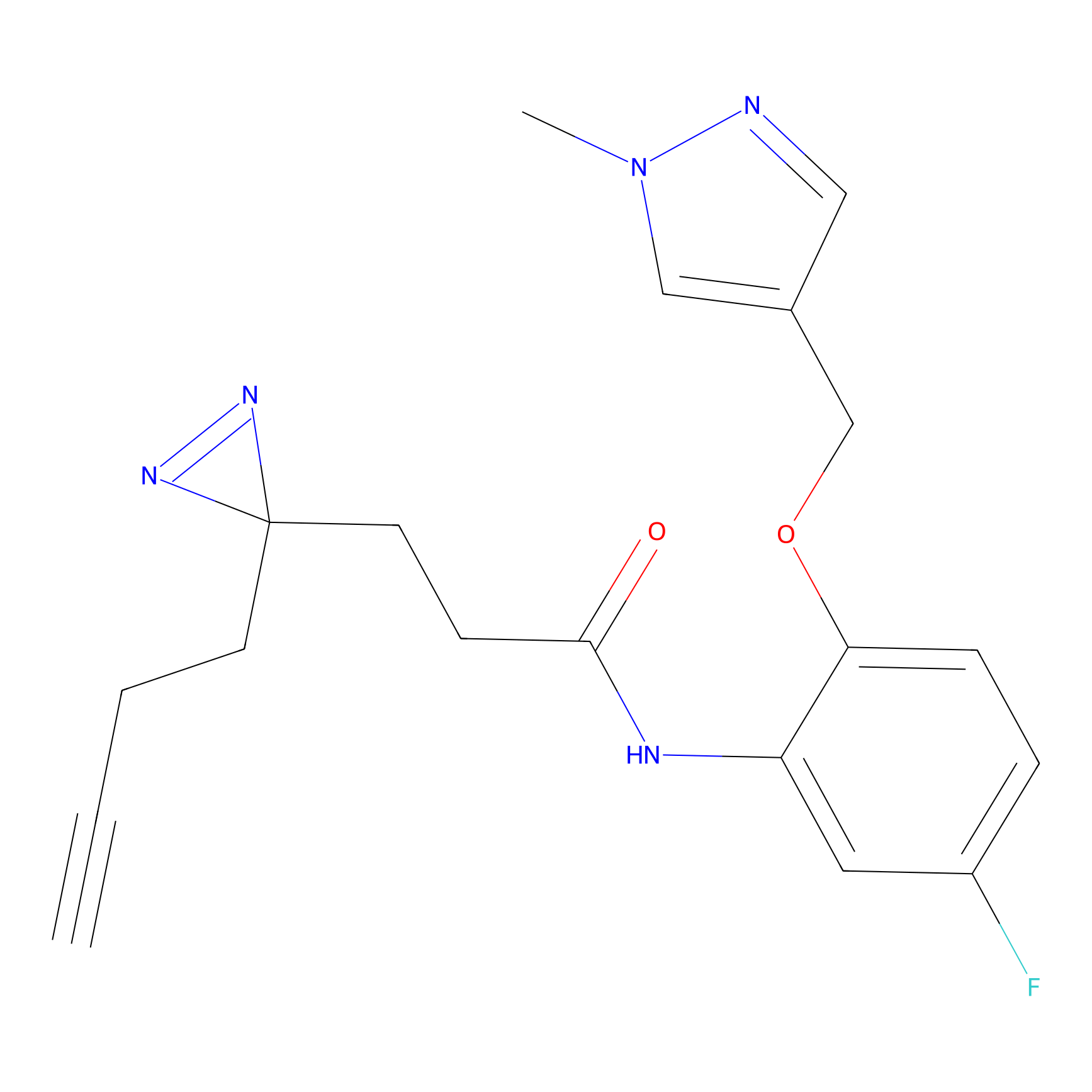
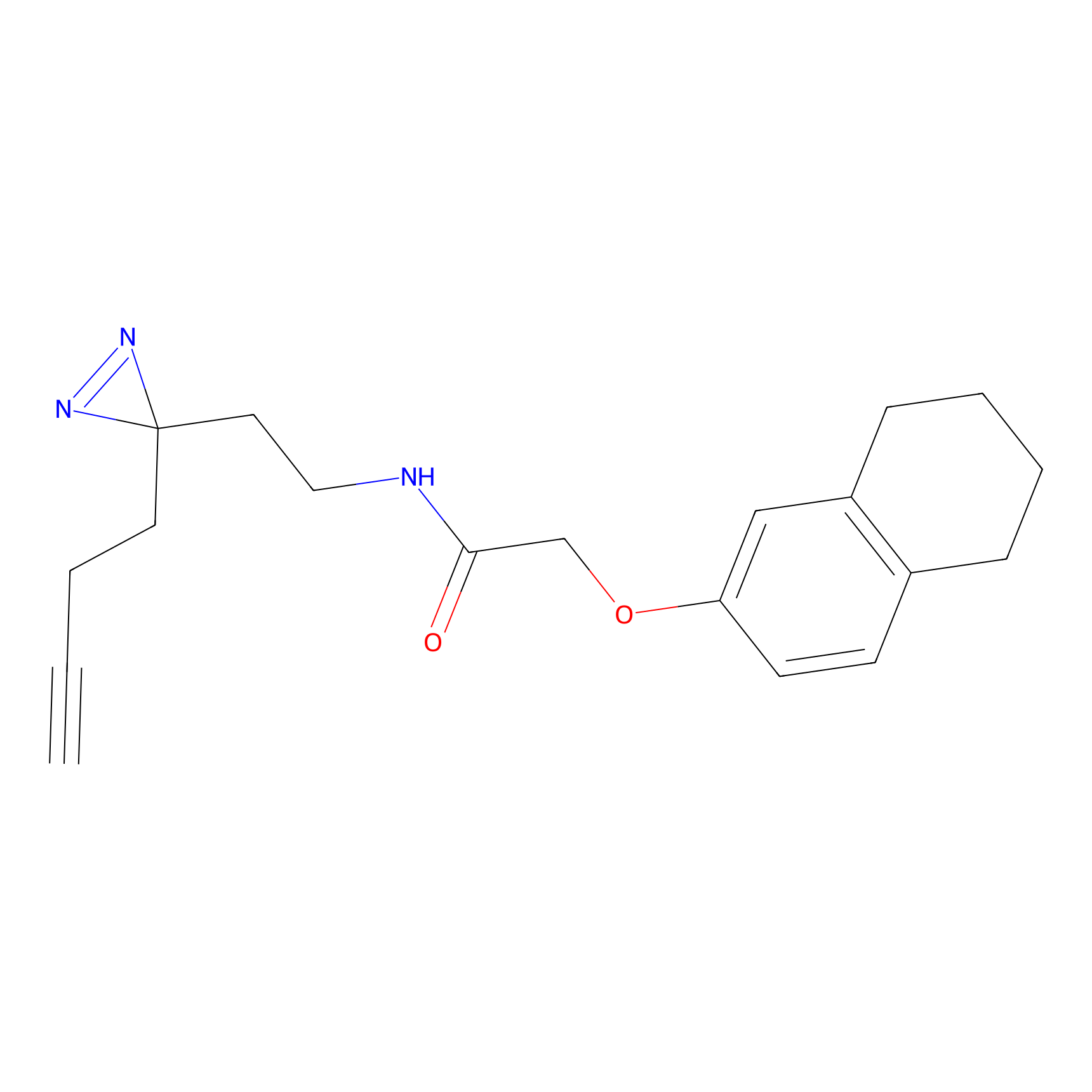
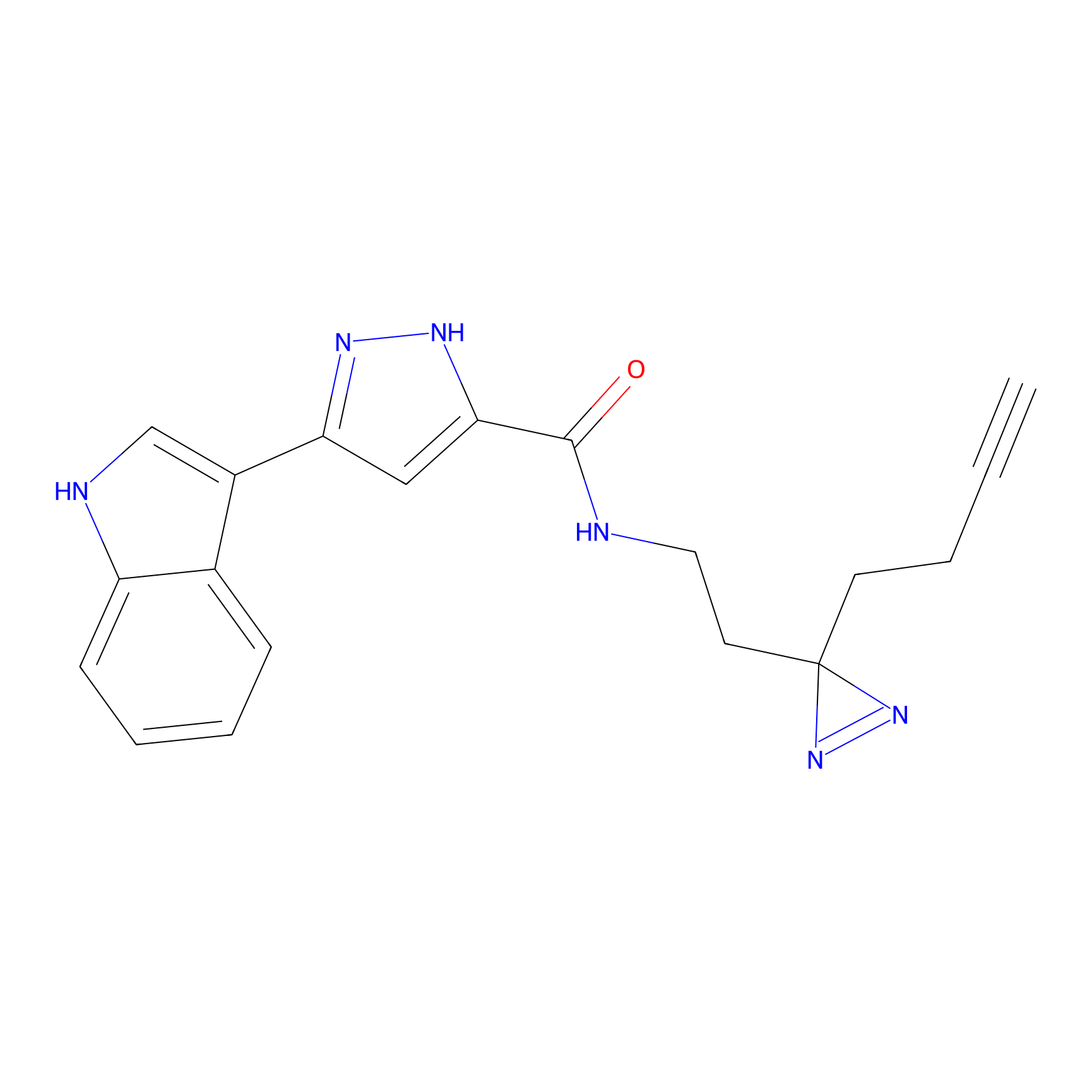
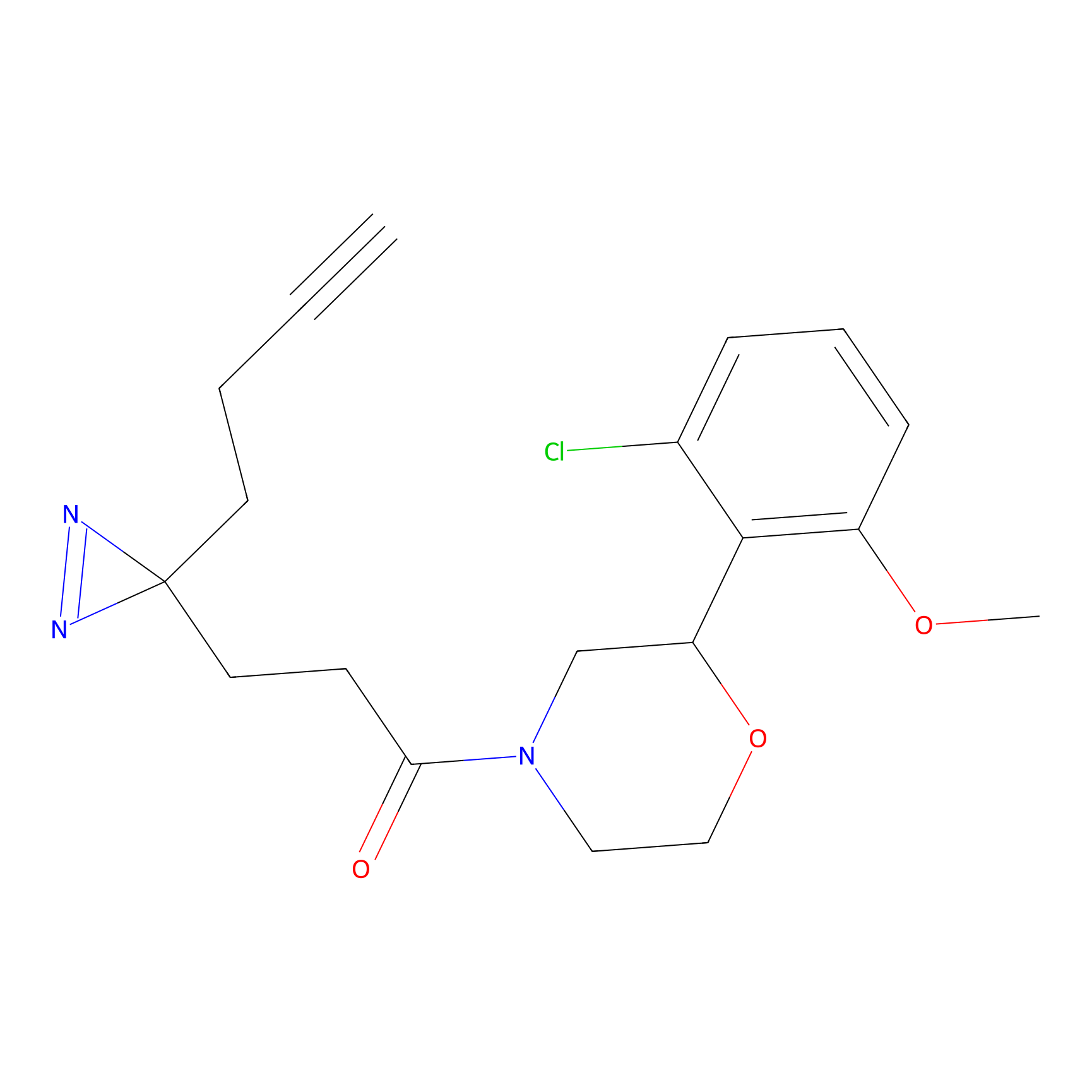
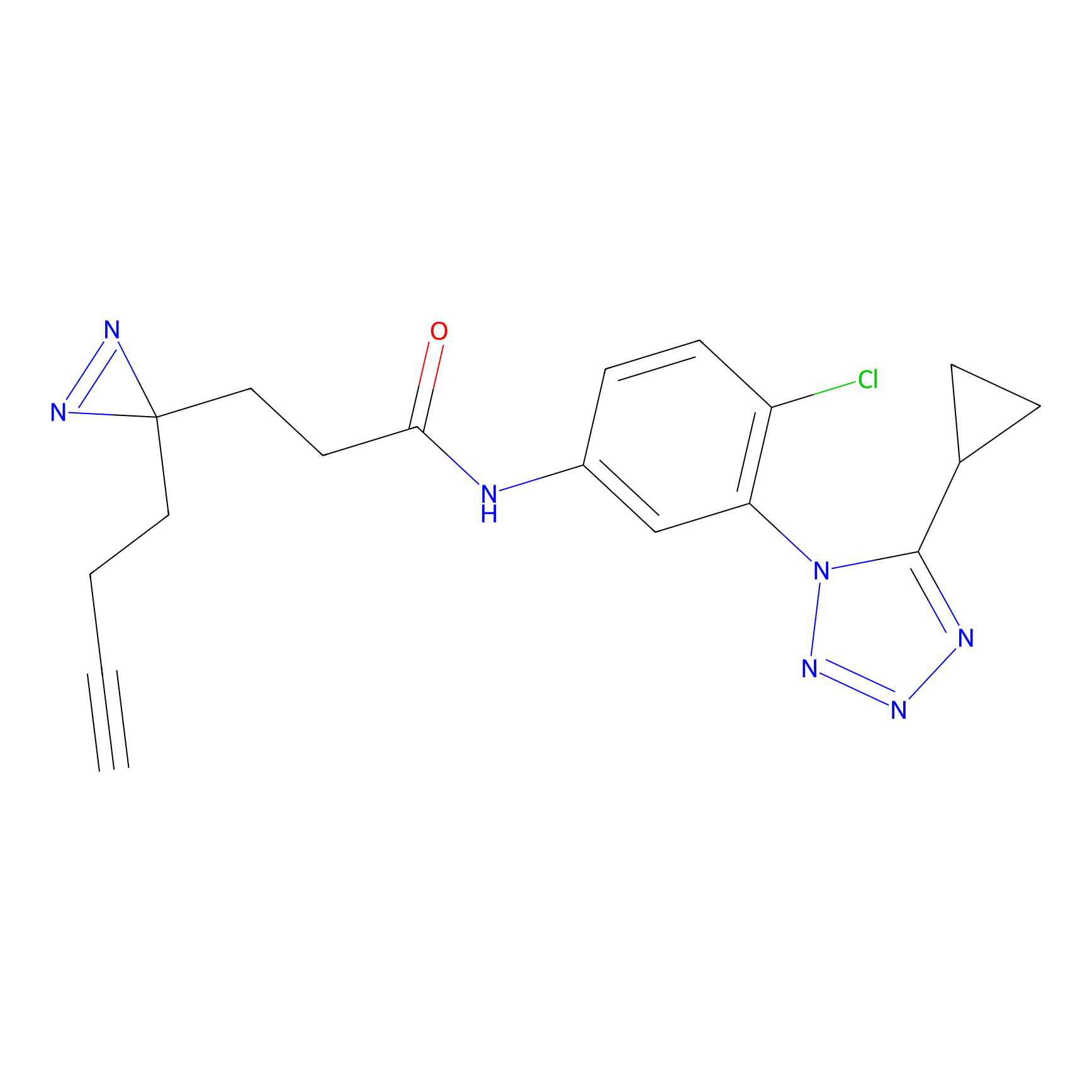
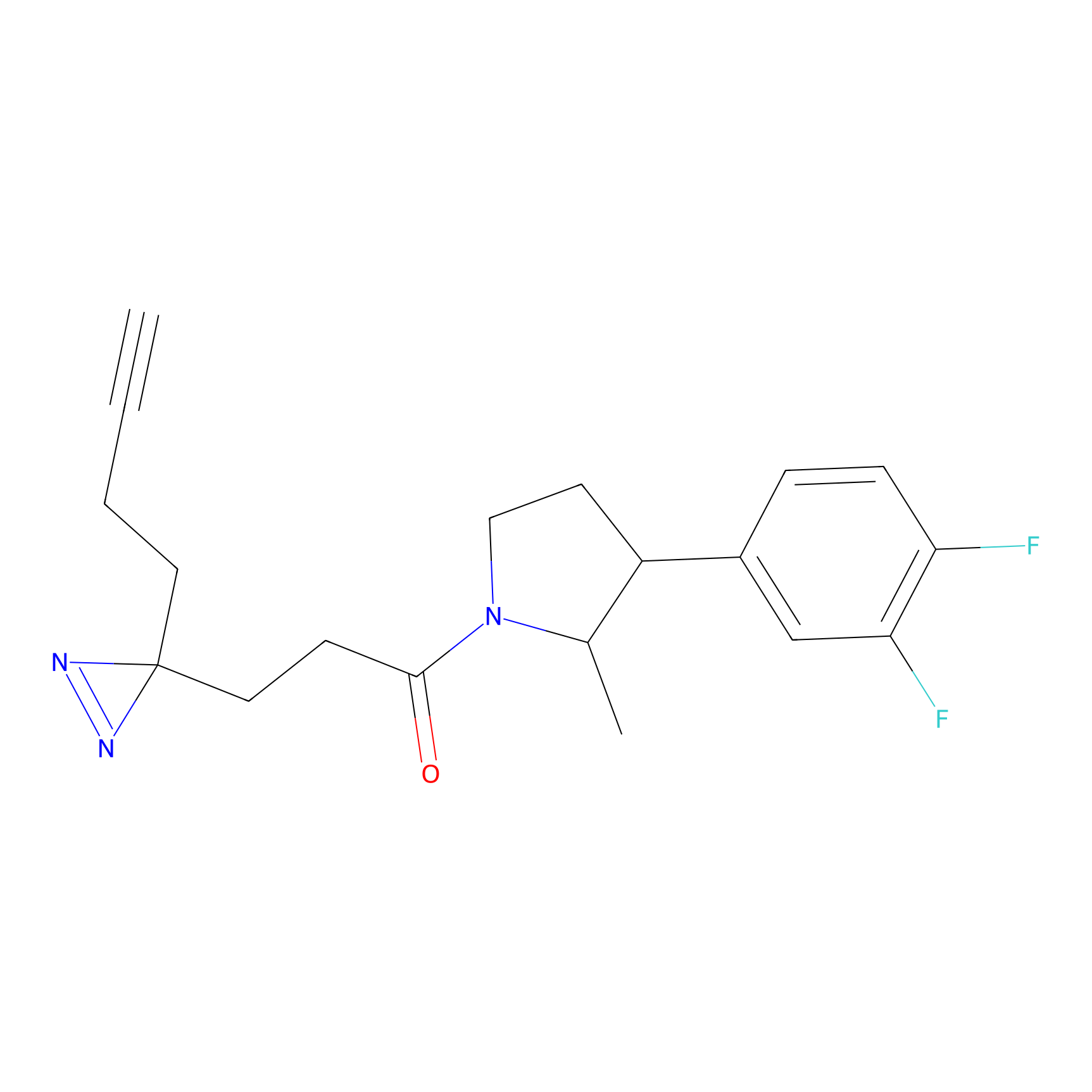
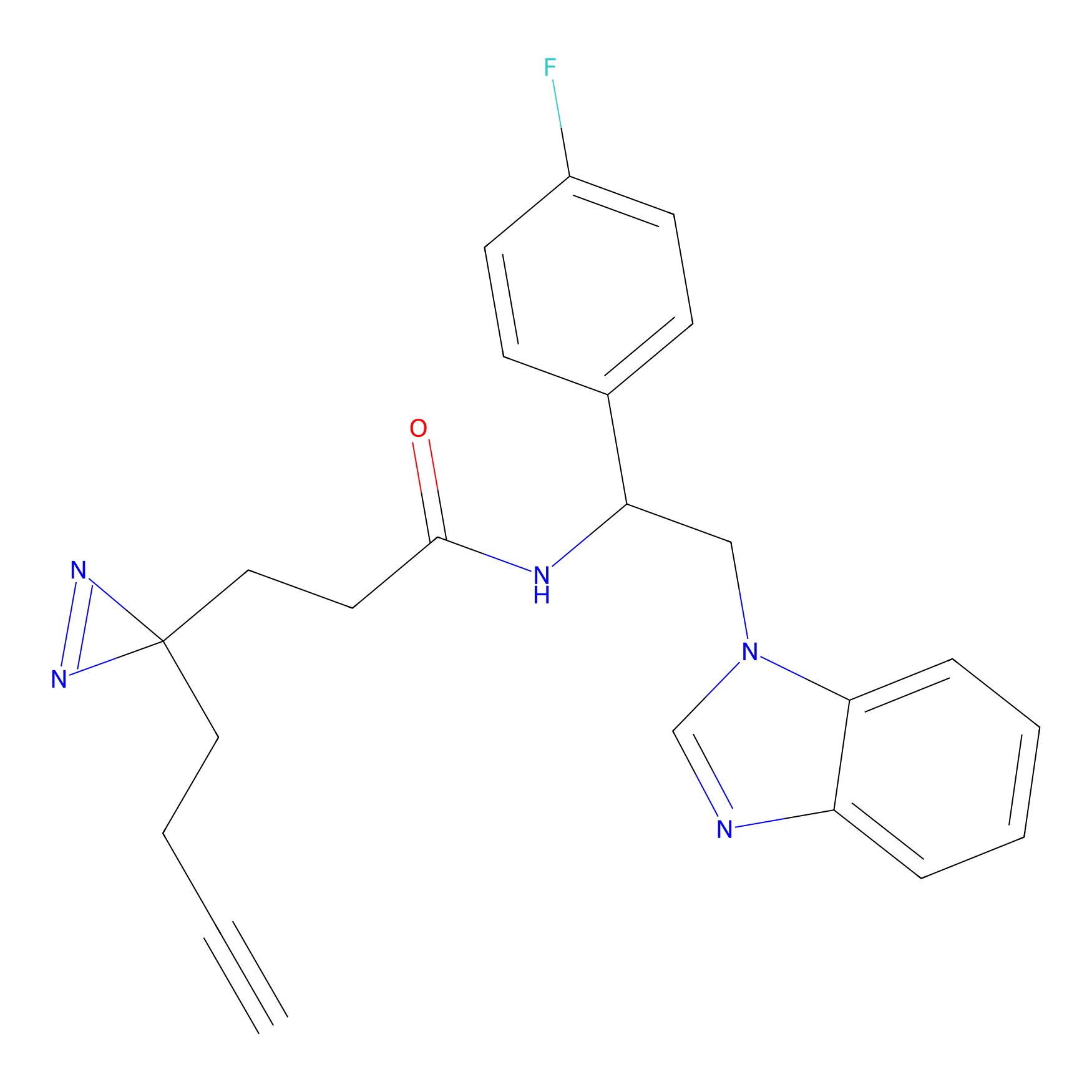
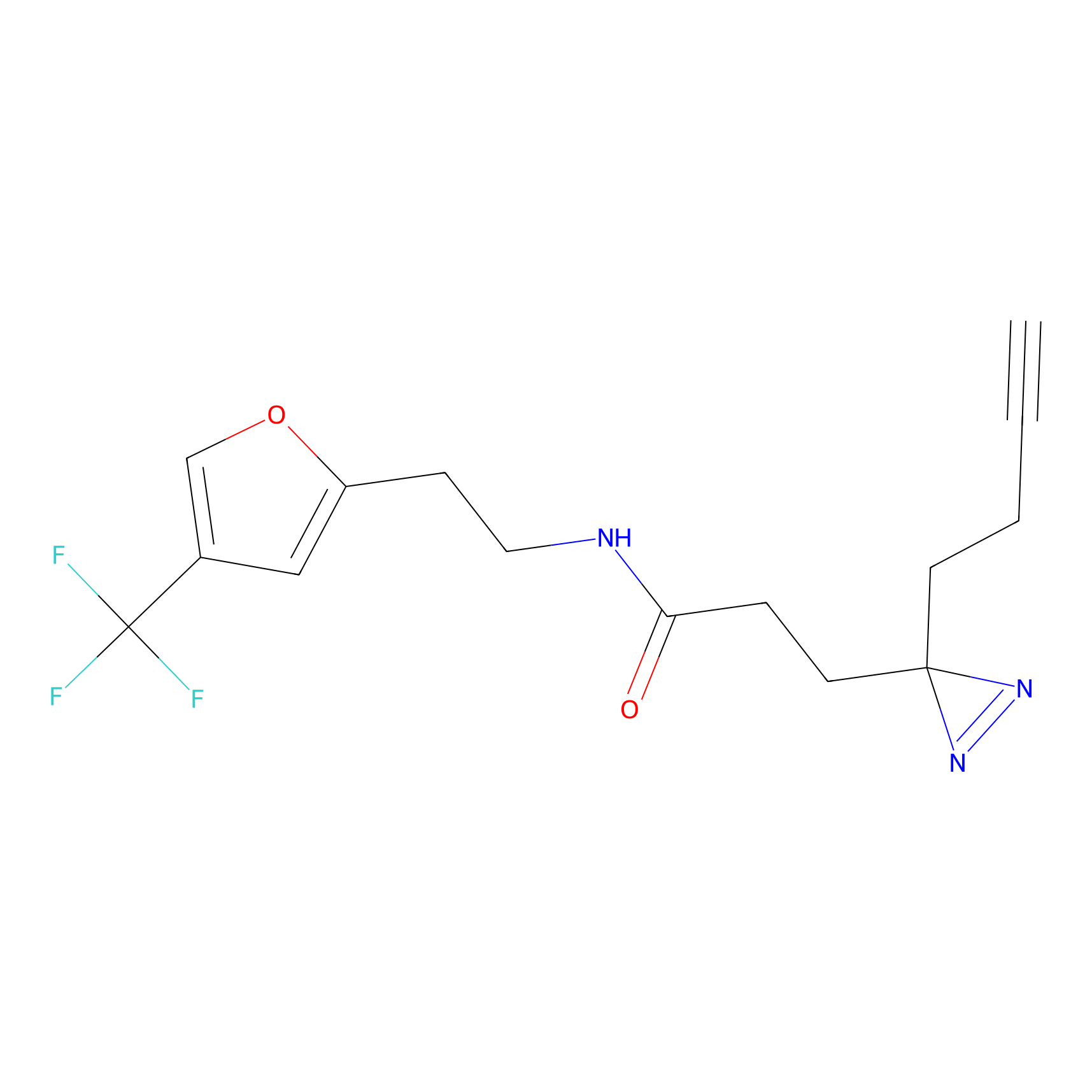
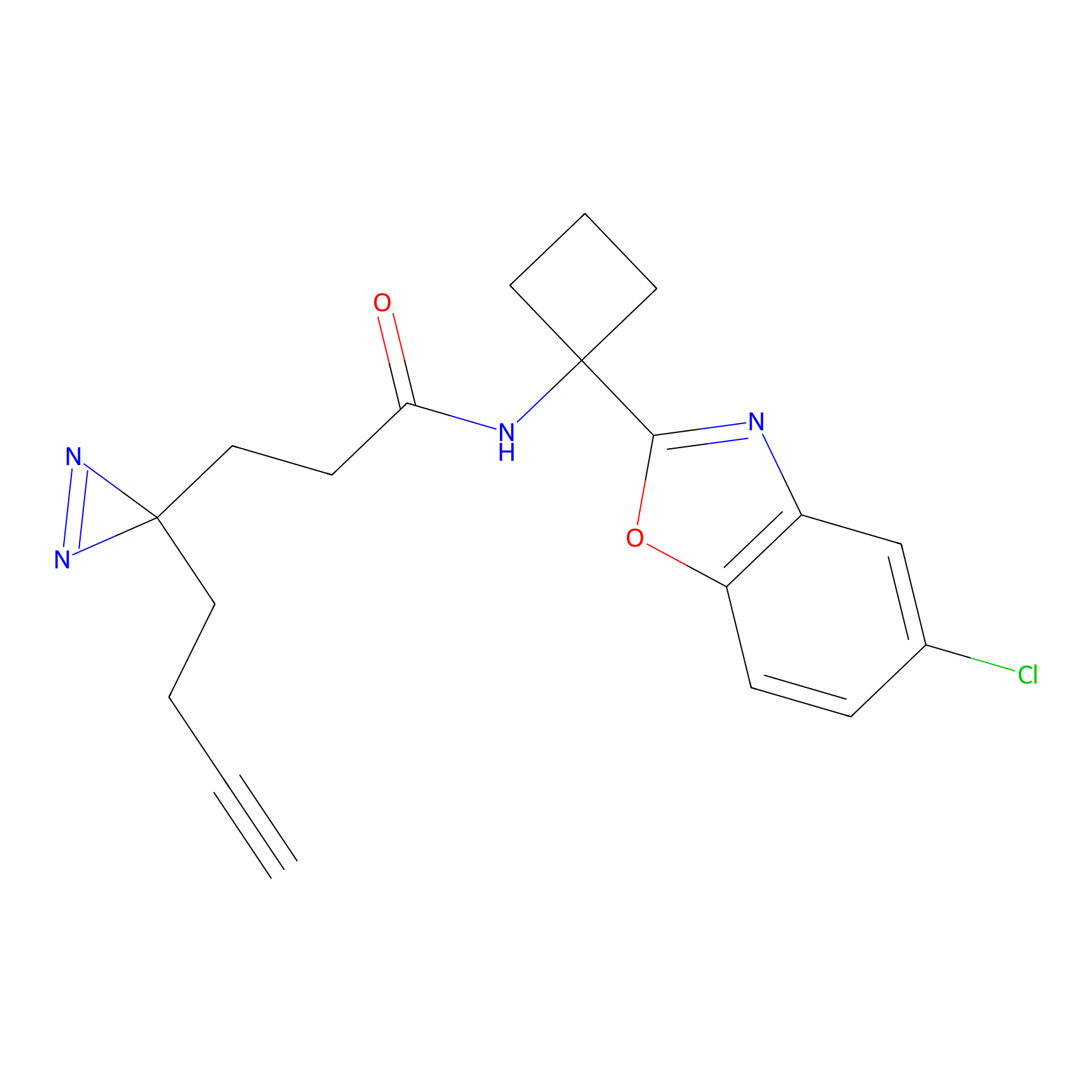
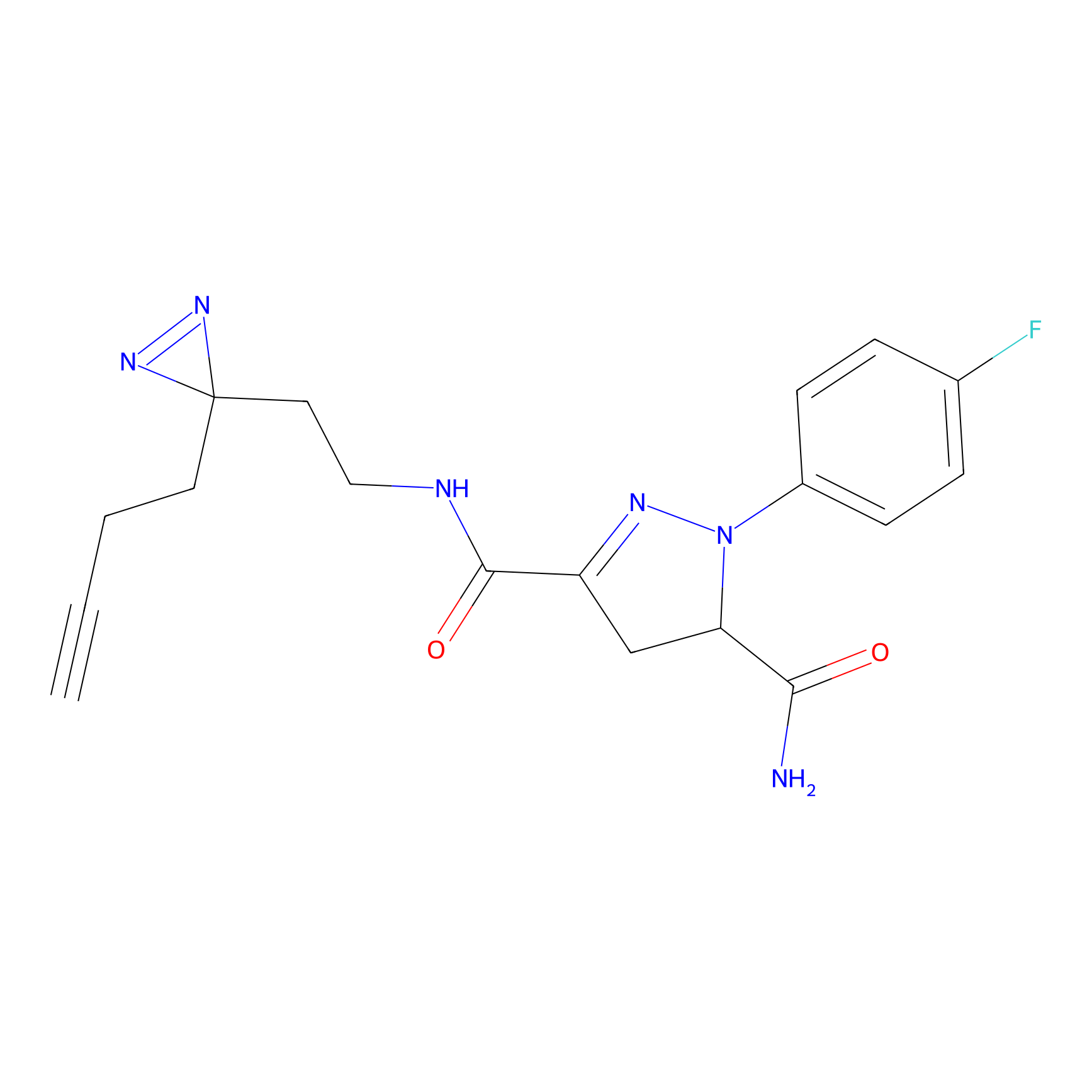
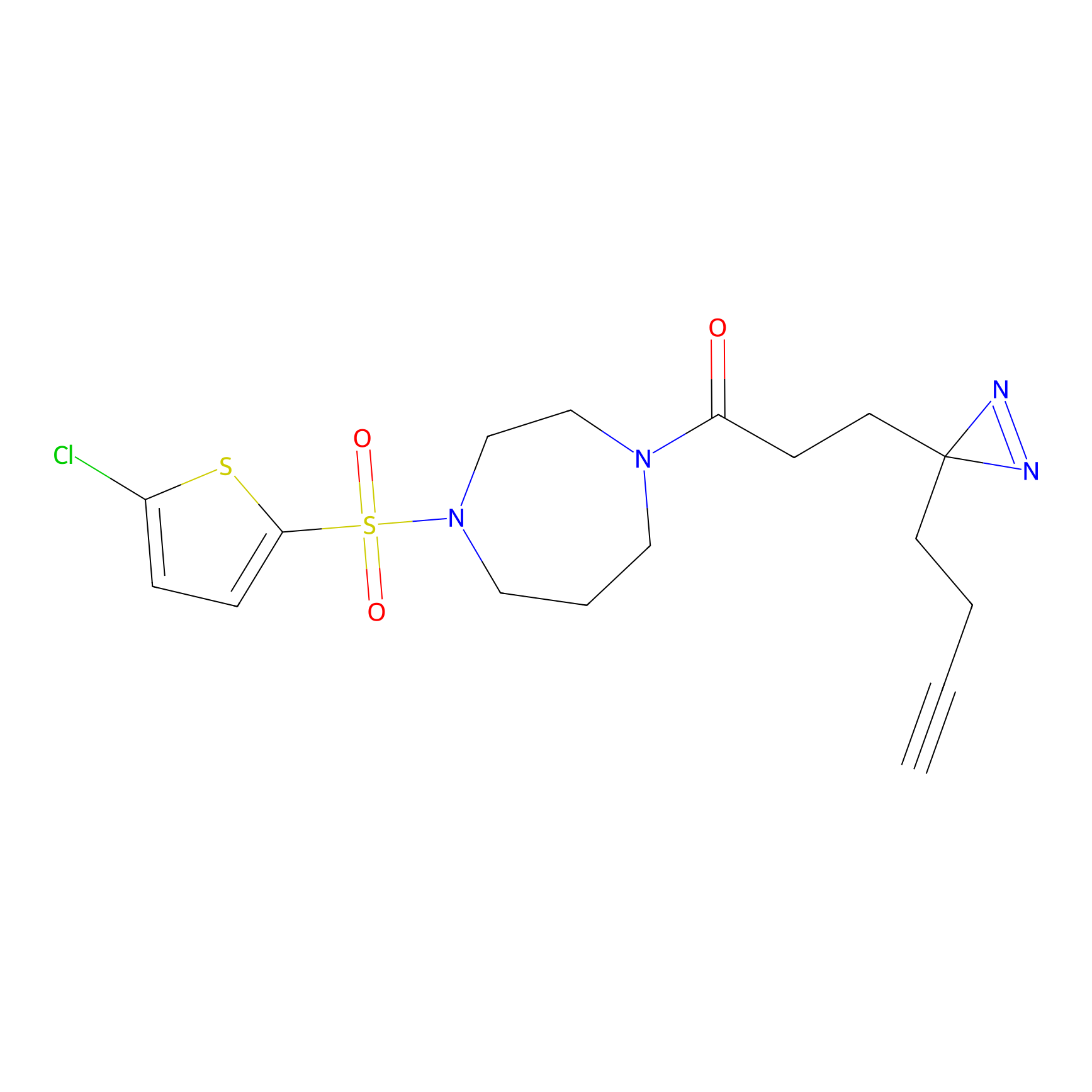
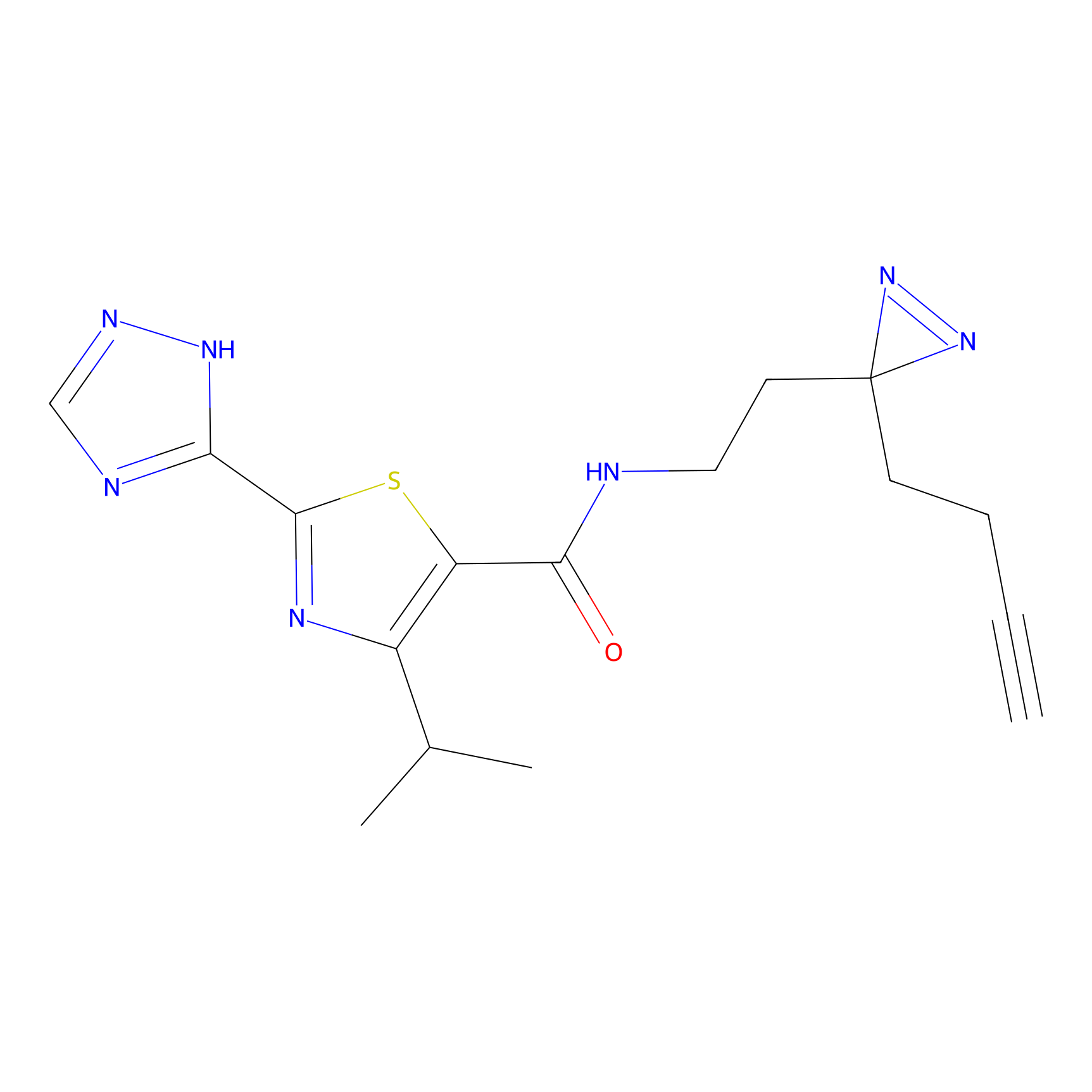
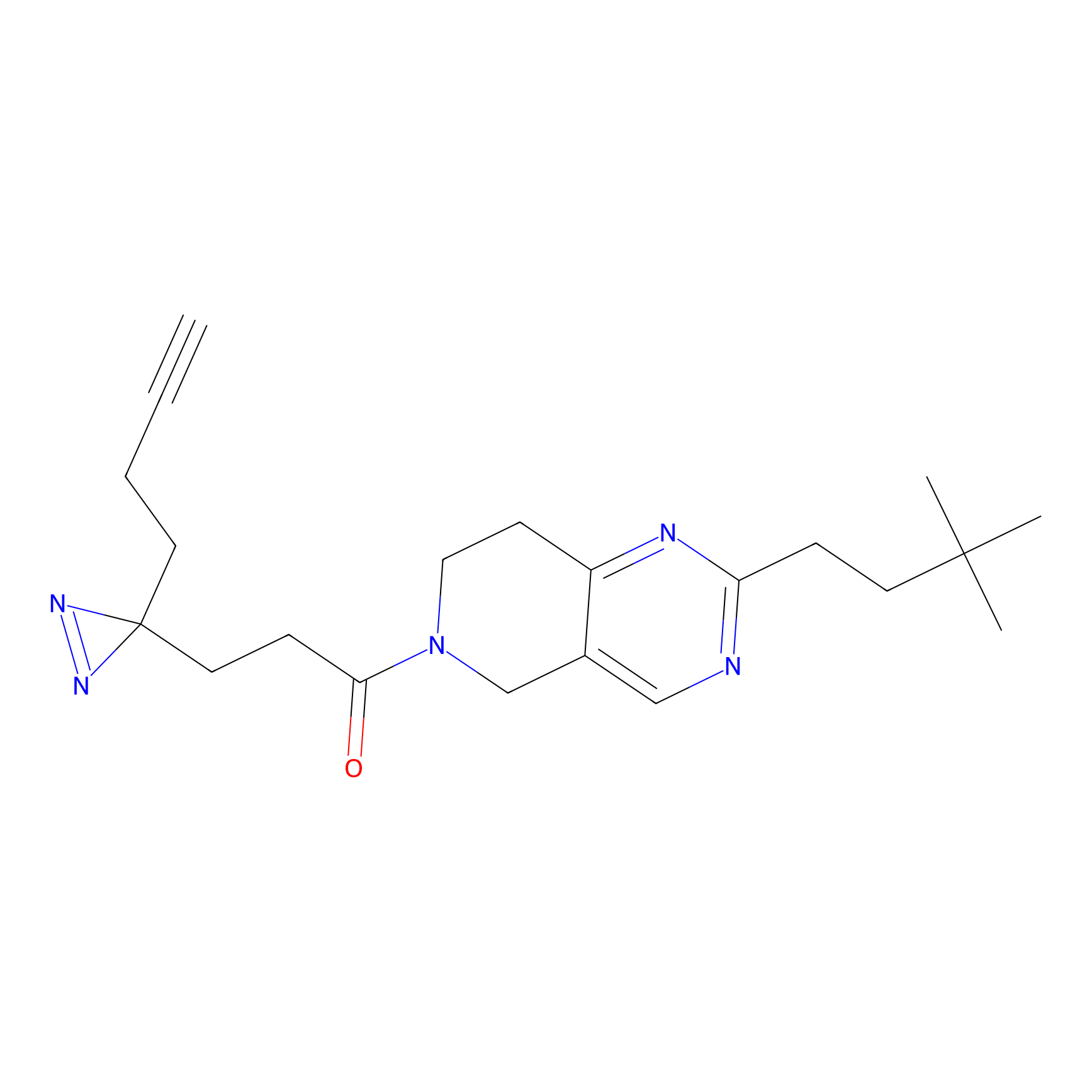
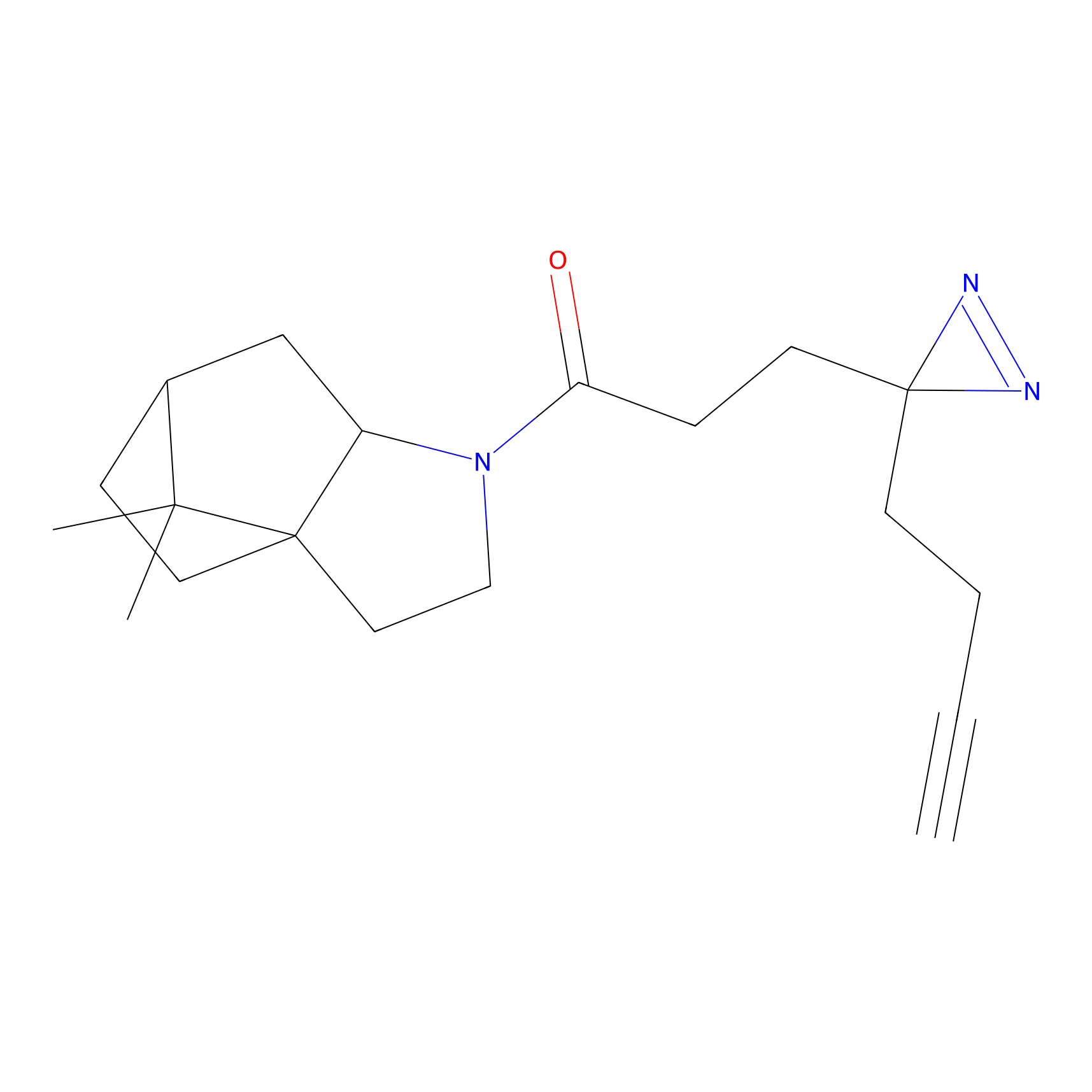
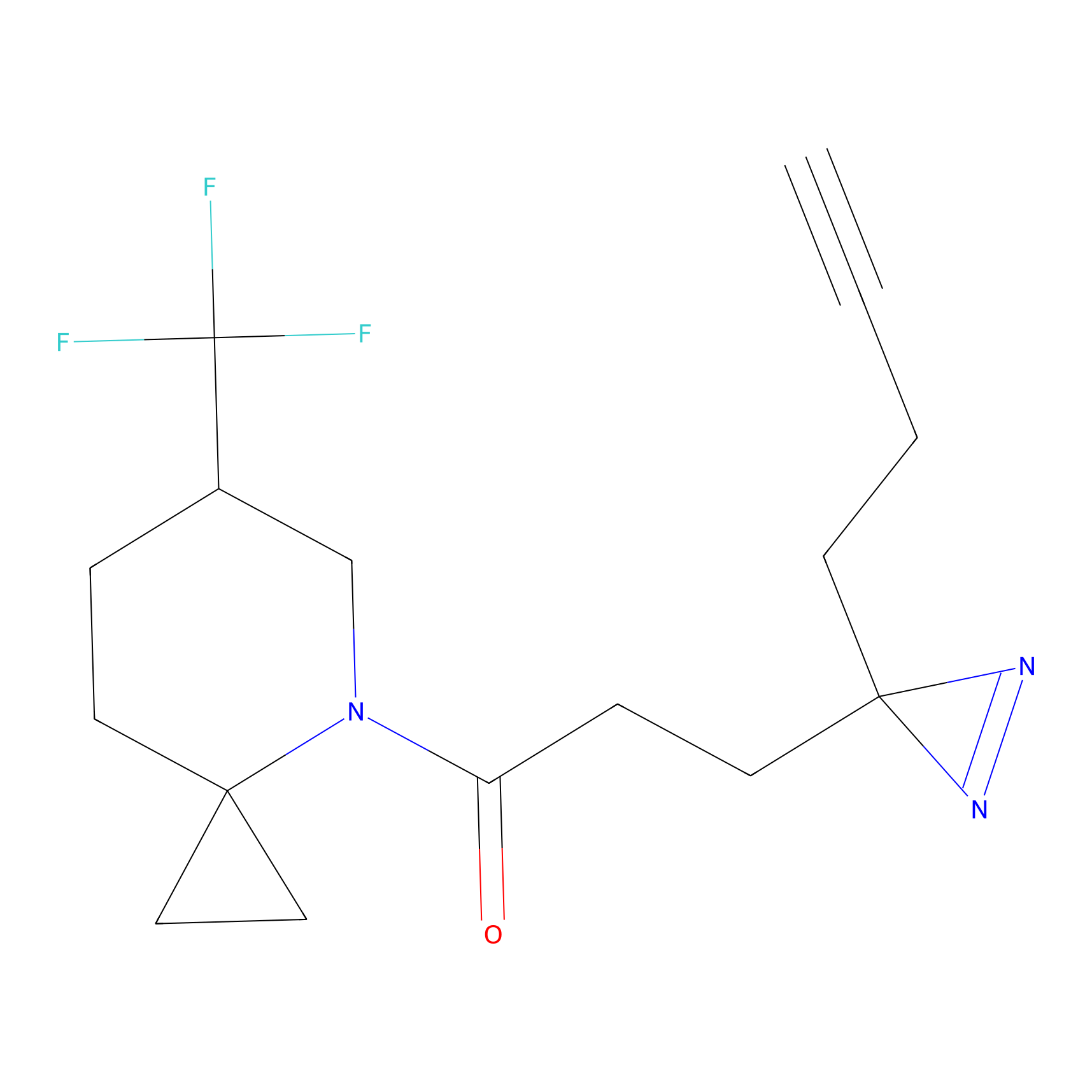
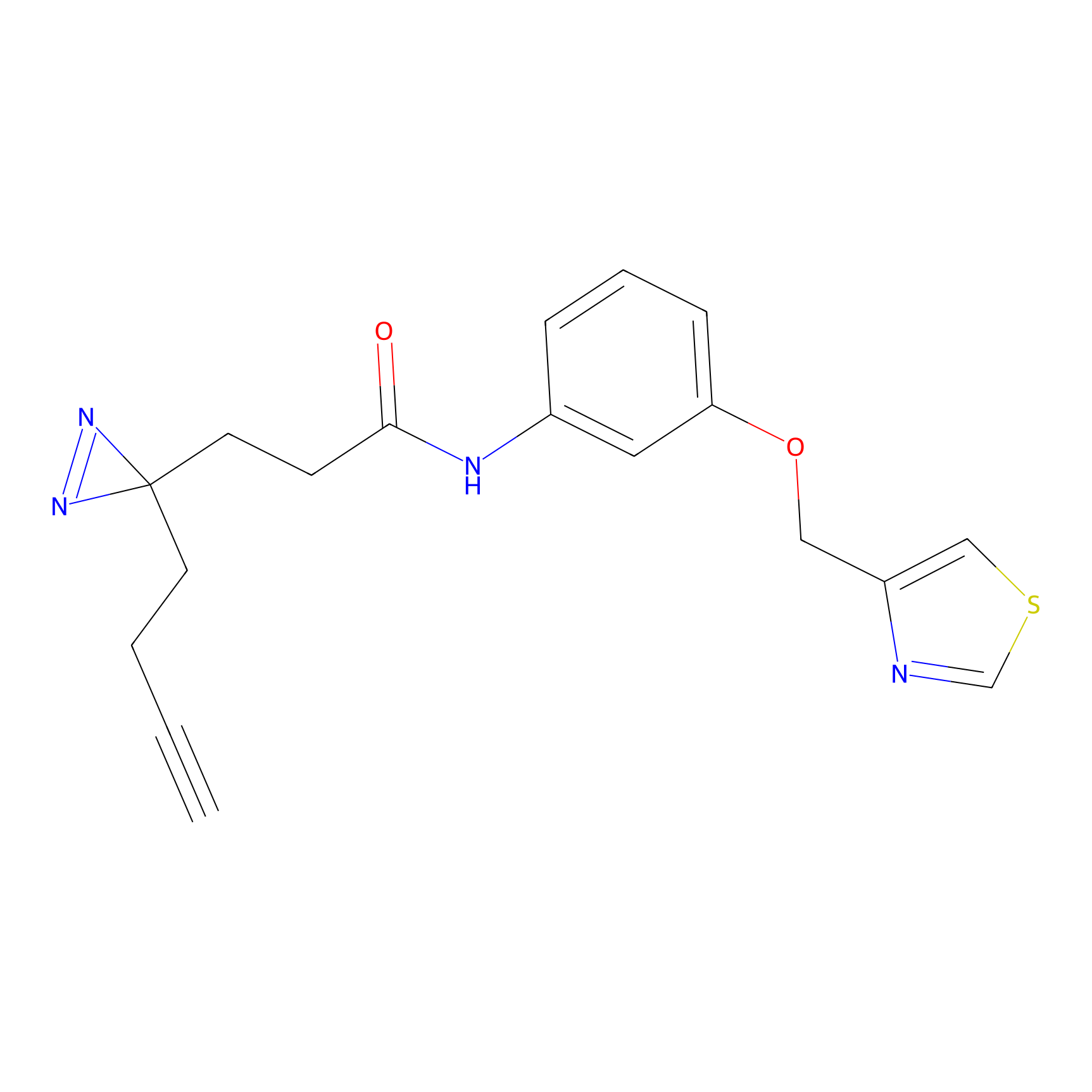
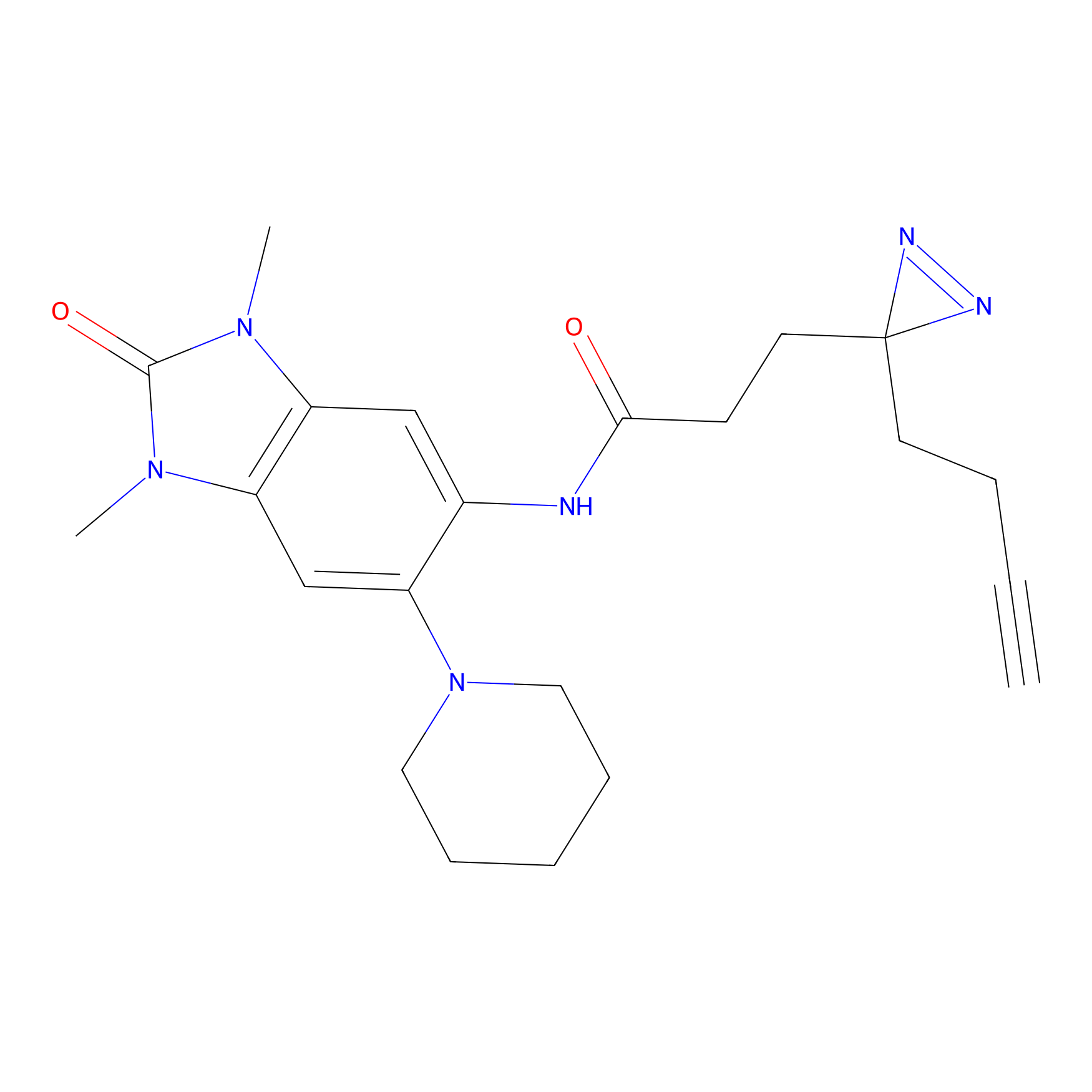
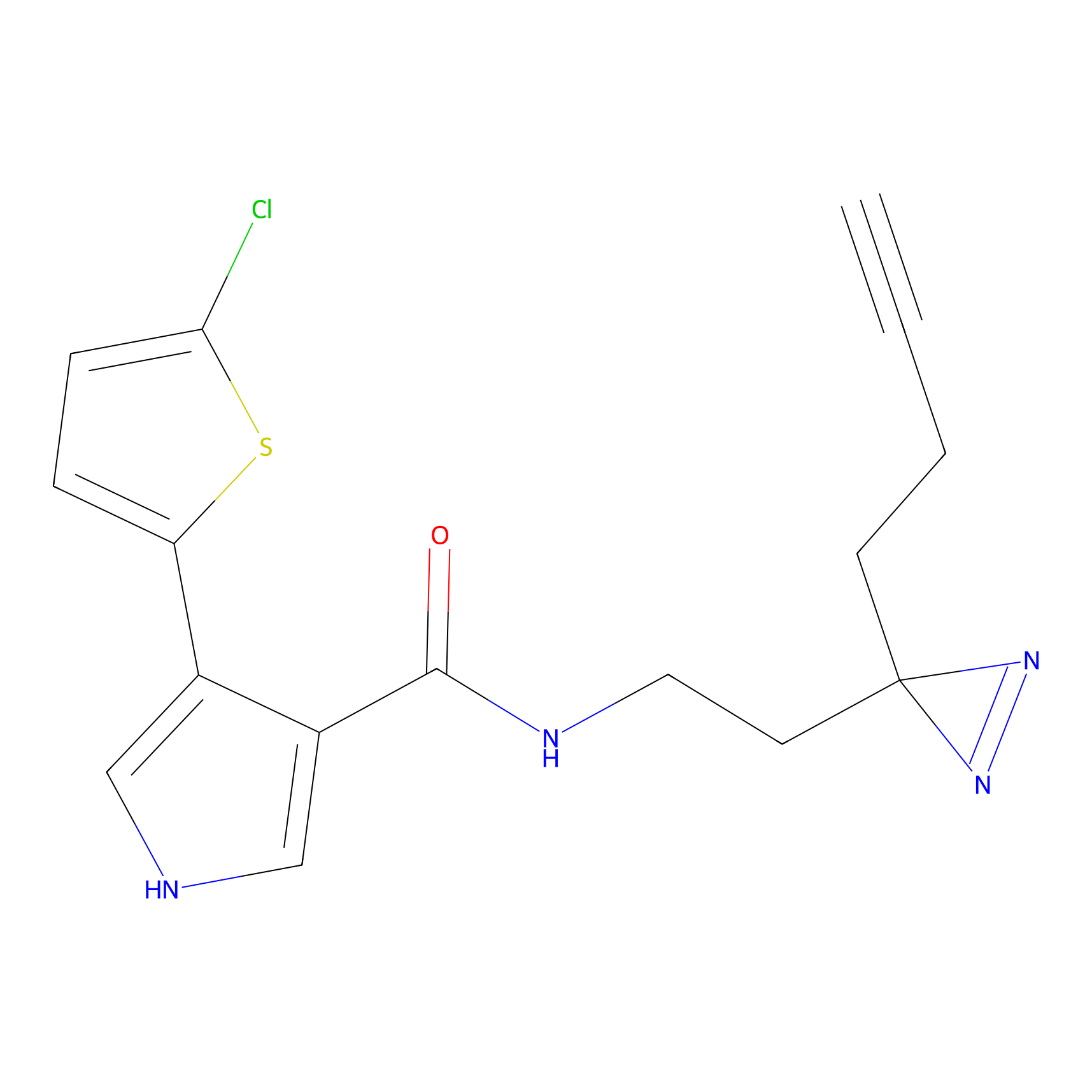
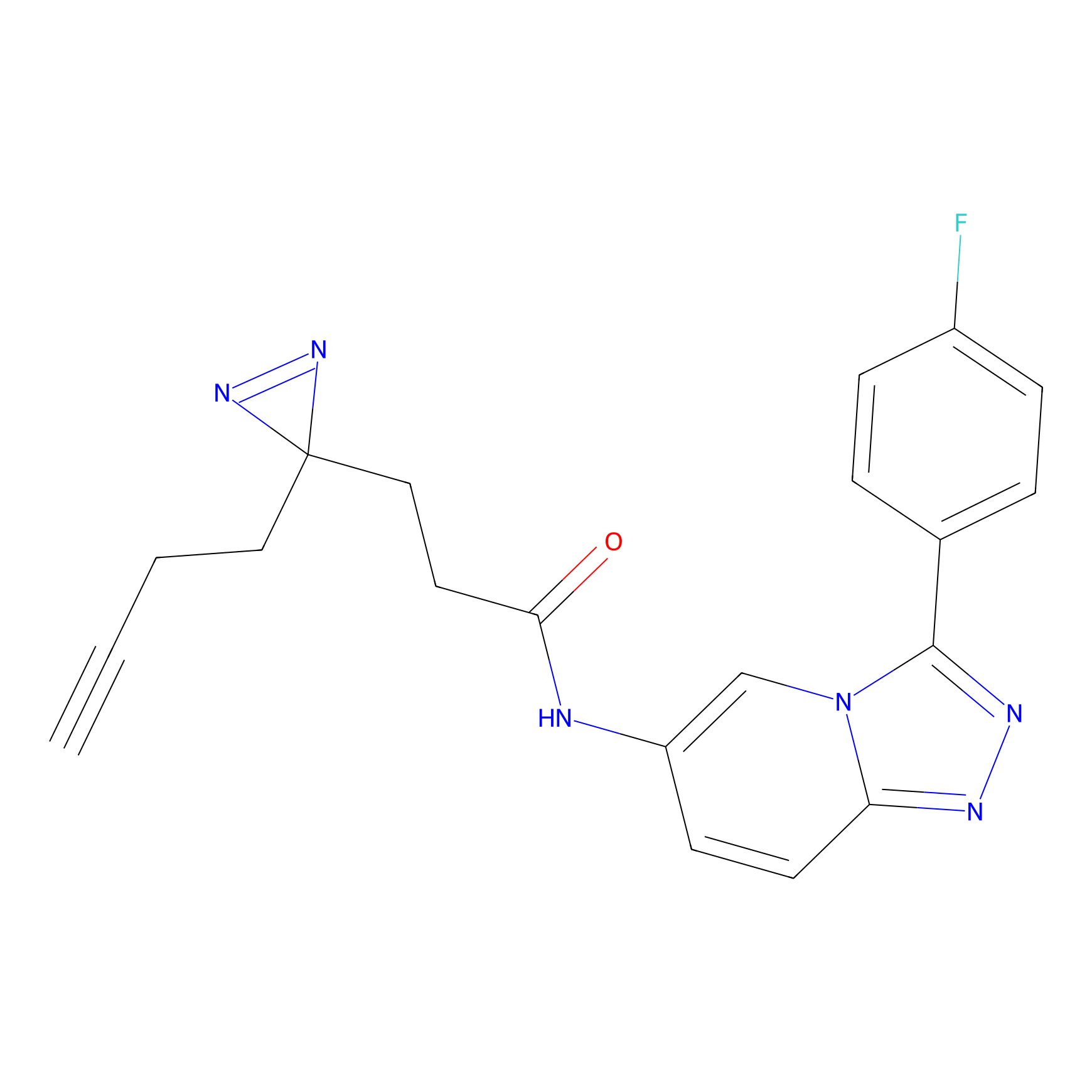
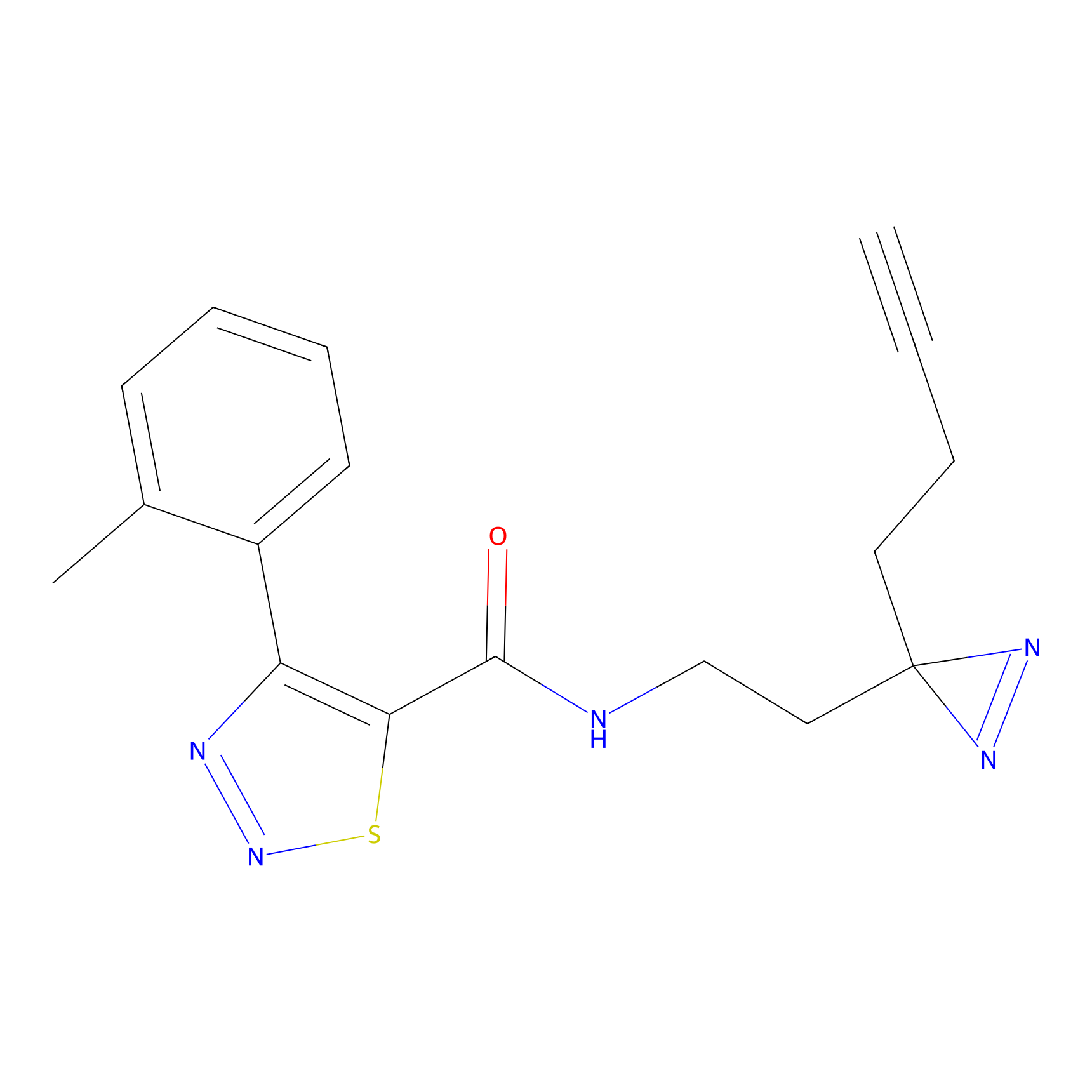
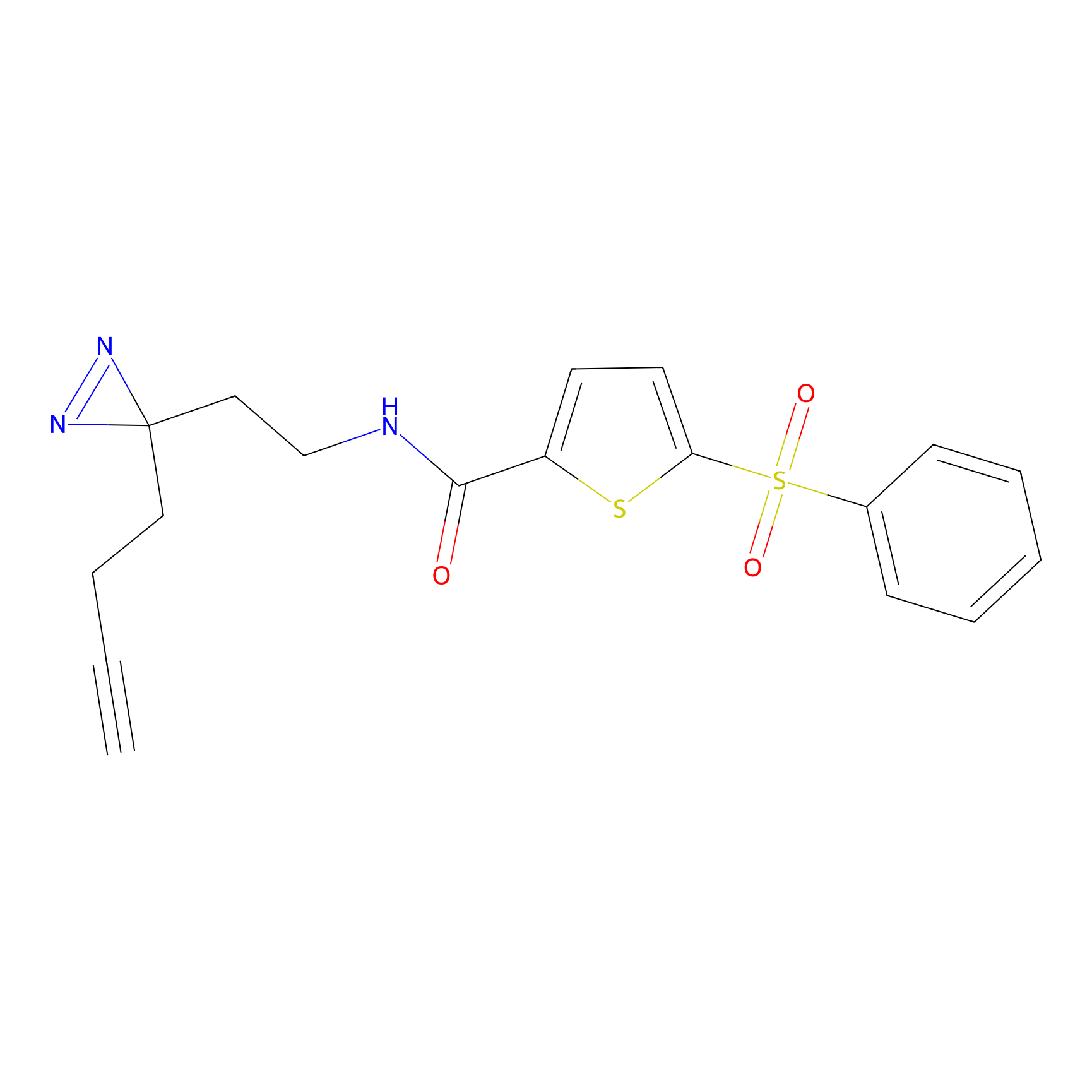
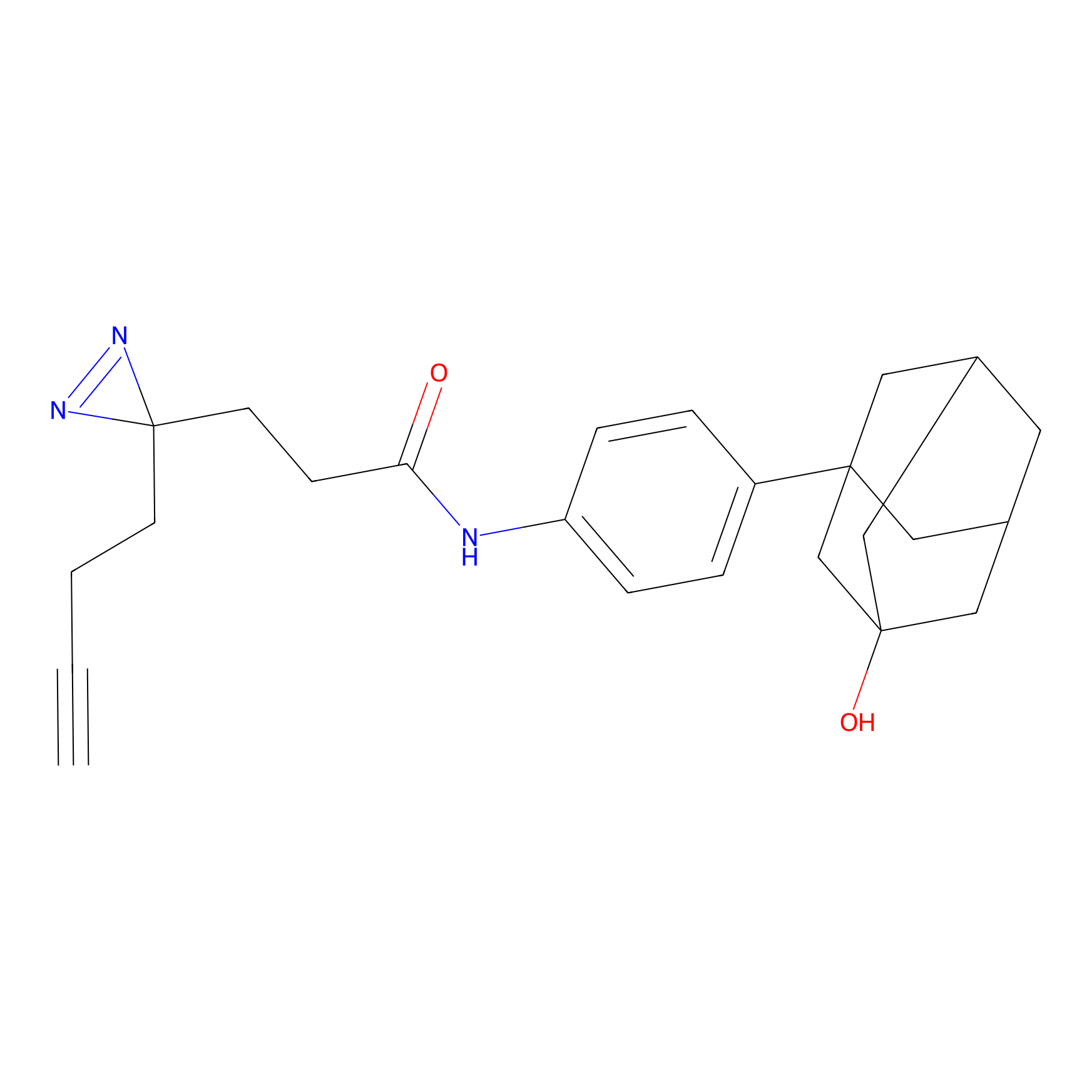
Details of the Target
General Information of Target
| Target ID | LDTP13983 | |||||
|---|---|---|---|---|---|---|
| Target Name | Mitochondrial import inner membrane translocase subunit TIM16 (PAM16) | |||||
| Gene Name | PAM16 | |||||
| Gene ID | 51025 | |||||
| Synonyms |
MAGMAS; TIM16; TIMM16; Mitochondrial import inner membrane translocase subunit TIM16; Mitochondria-associated granulocyte macrophage CSF-signaling molecule; Presequence translocated-associated motor subunit PAM16
|
|||||
| 3D Structure | ||||||
| Sequence |
MEAVLNELVSVEDLLKFEKKFQSEKAAGSVSKSTQFEYAWCLVRSKYNDDIRKGIVLLEE
LLPKGSKEEQRDYVFYLAVGNYRLKEYEKALKYVRGLLQTEPQNNQAKELERLIDKAMKK DGLVGMAIVGGMALGVAGLAGLIGLAVSKSKS |
|||||
| Target Bioclass |
Transporter and channel
|
|||||
| Family |
TIM16/PAM16 family
|
|||||
| Subcellular location |
Mitochondrion inner membrane
|
|||||
| Function | Regulates ATP-dependent protein translocation into the mitochondrial matrix. Inhibits DNAJC19 stimulation of HSPA9/Mortalin ATPase activity. | |||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
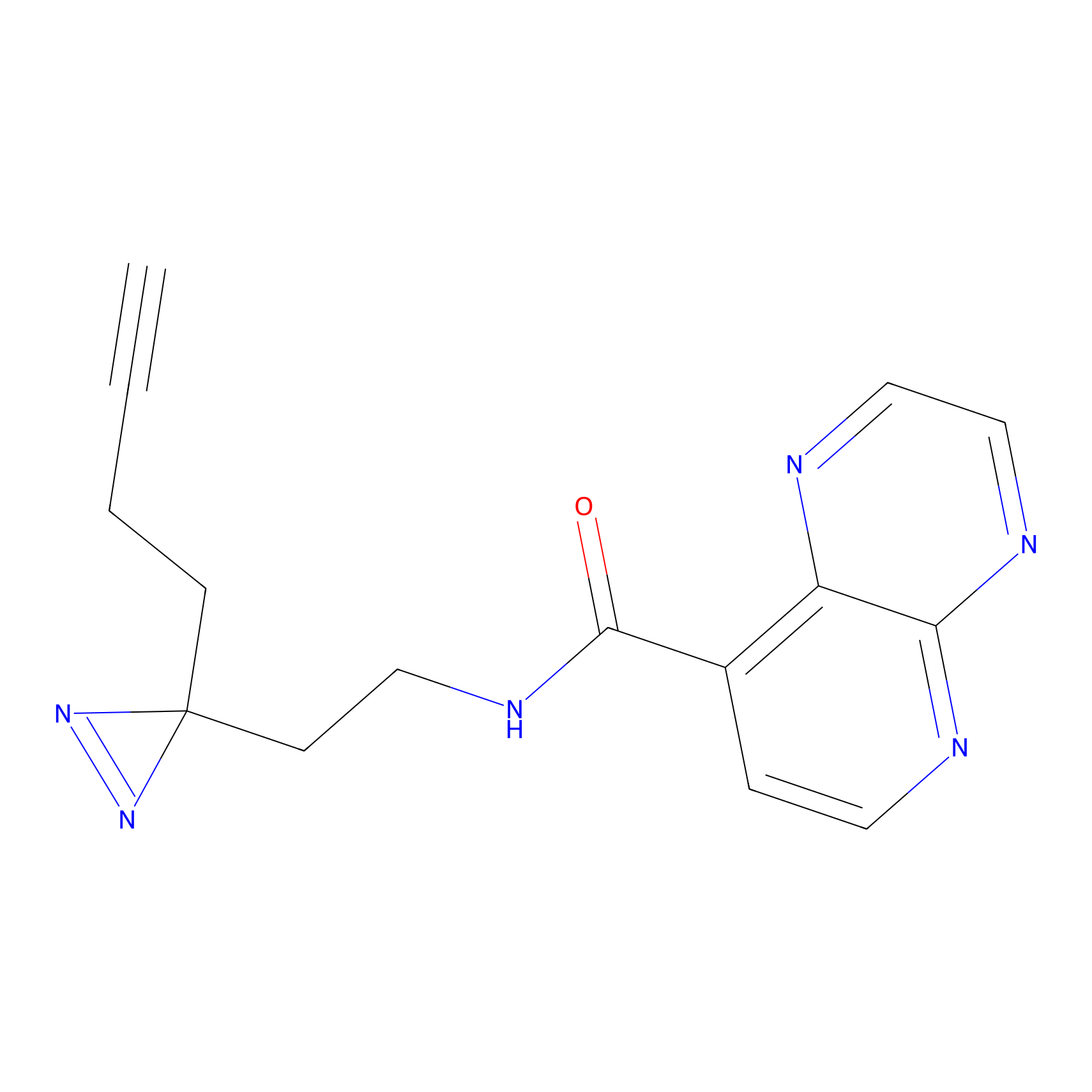
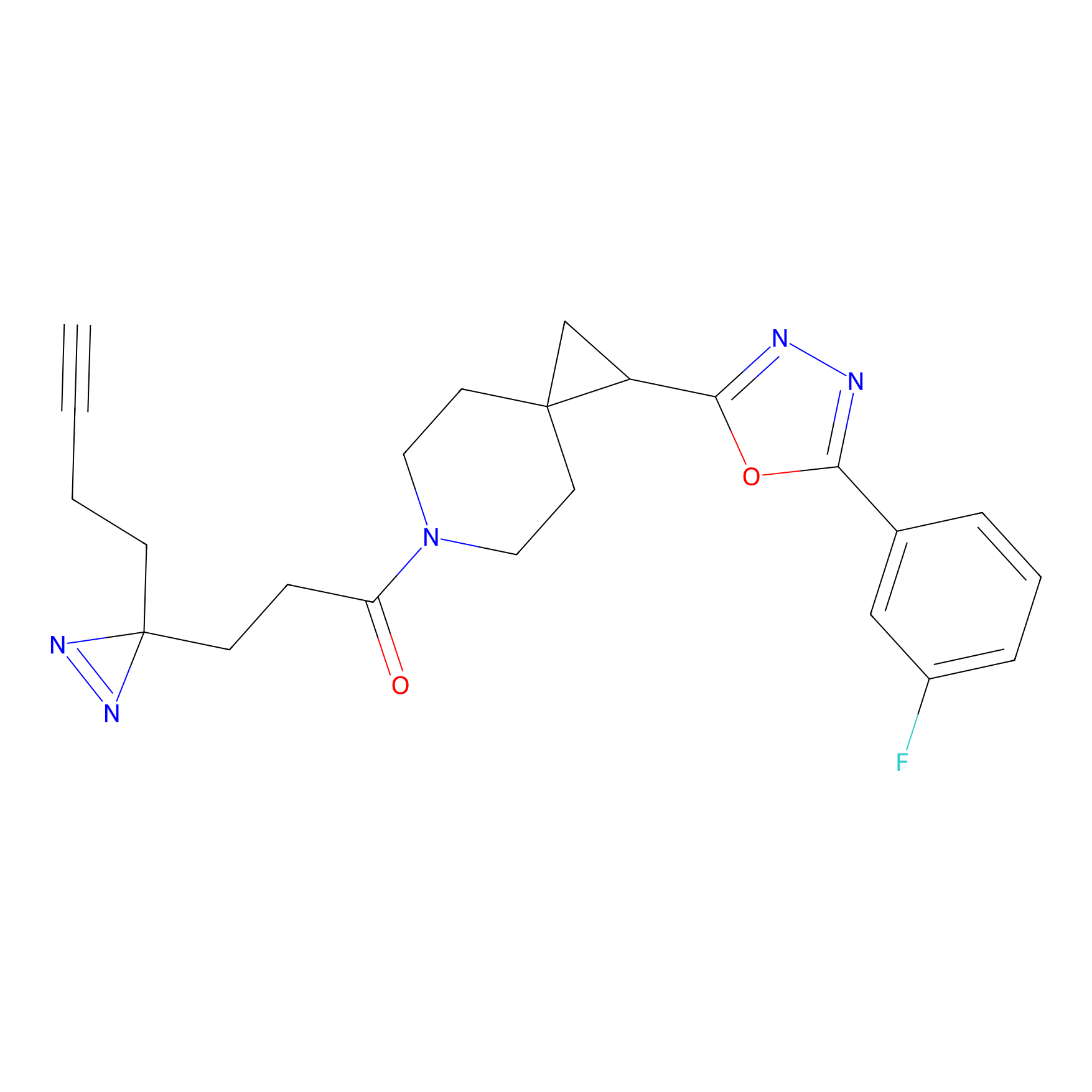
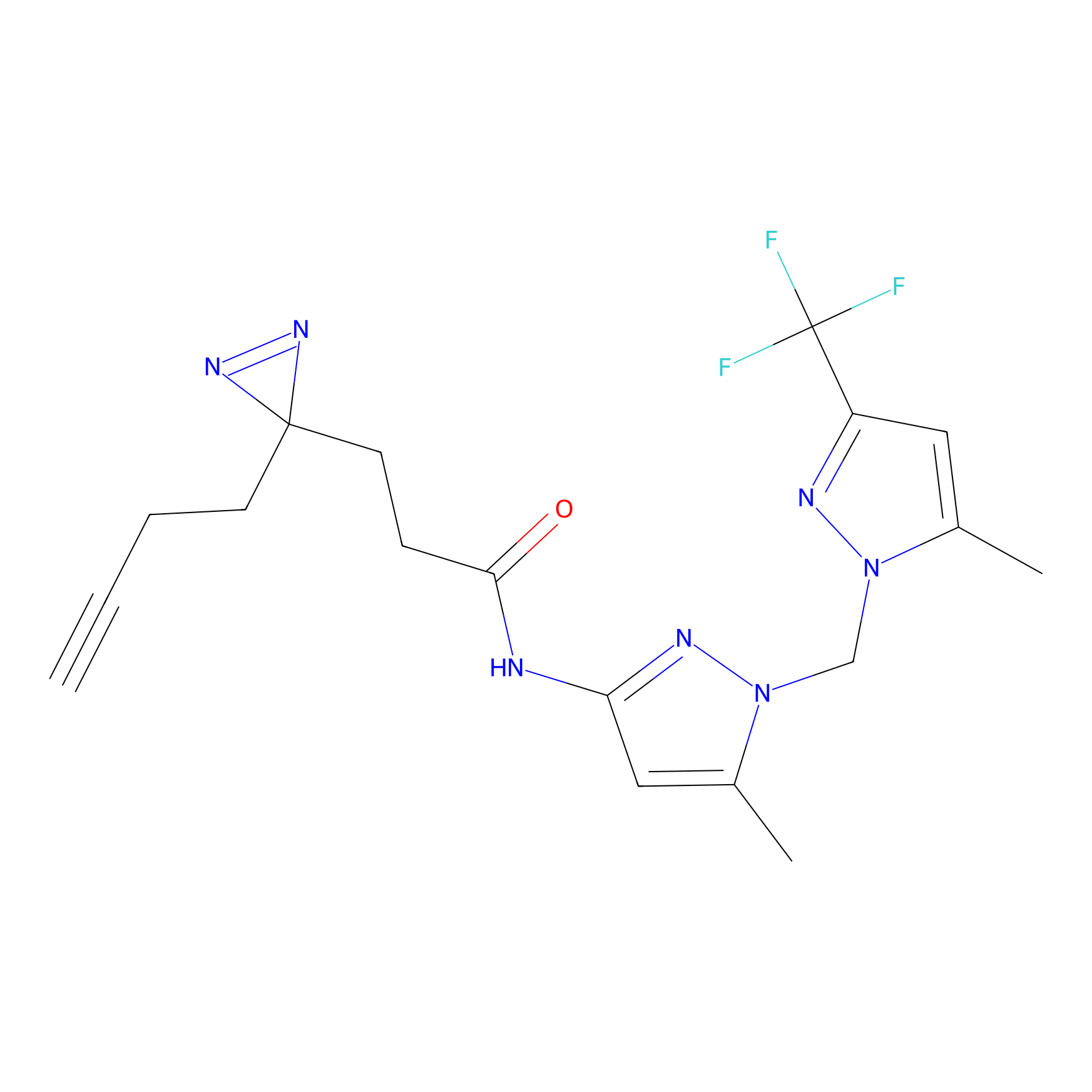
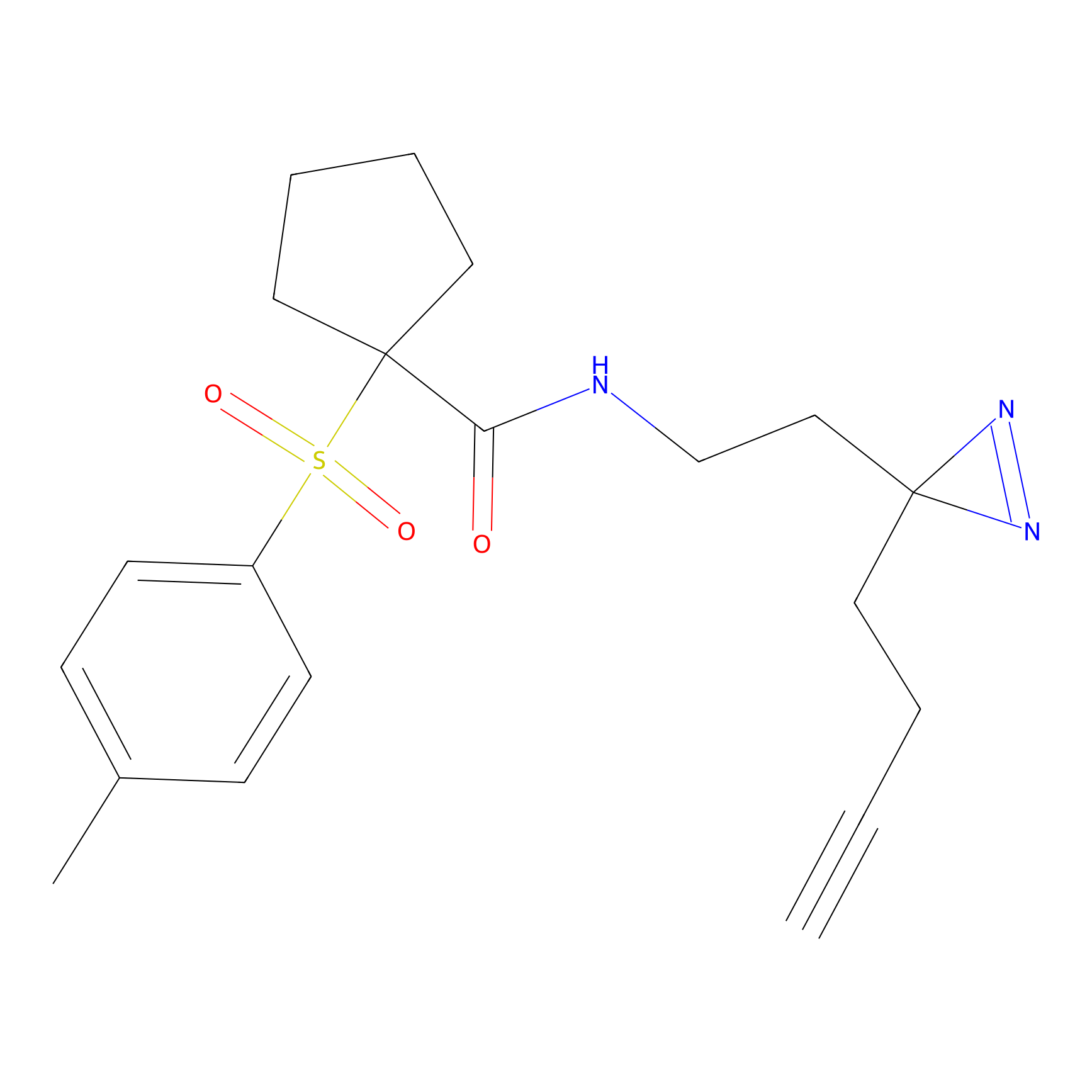
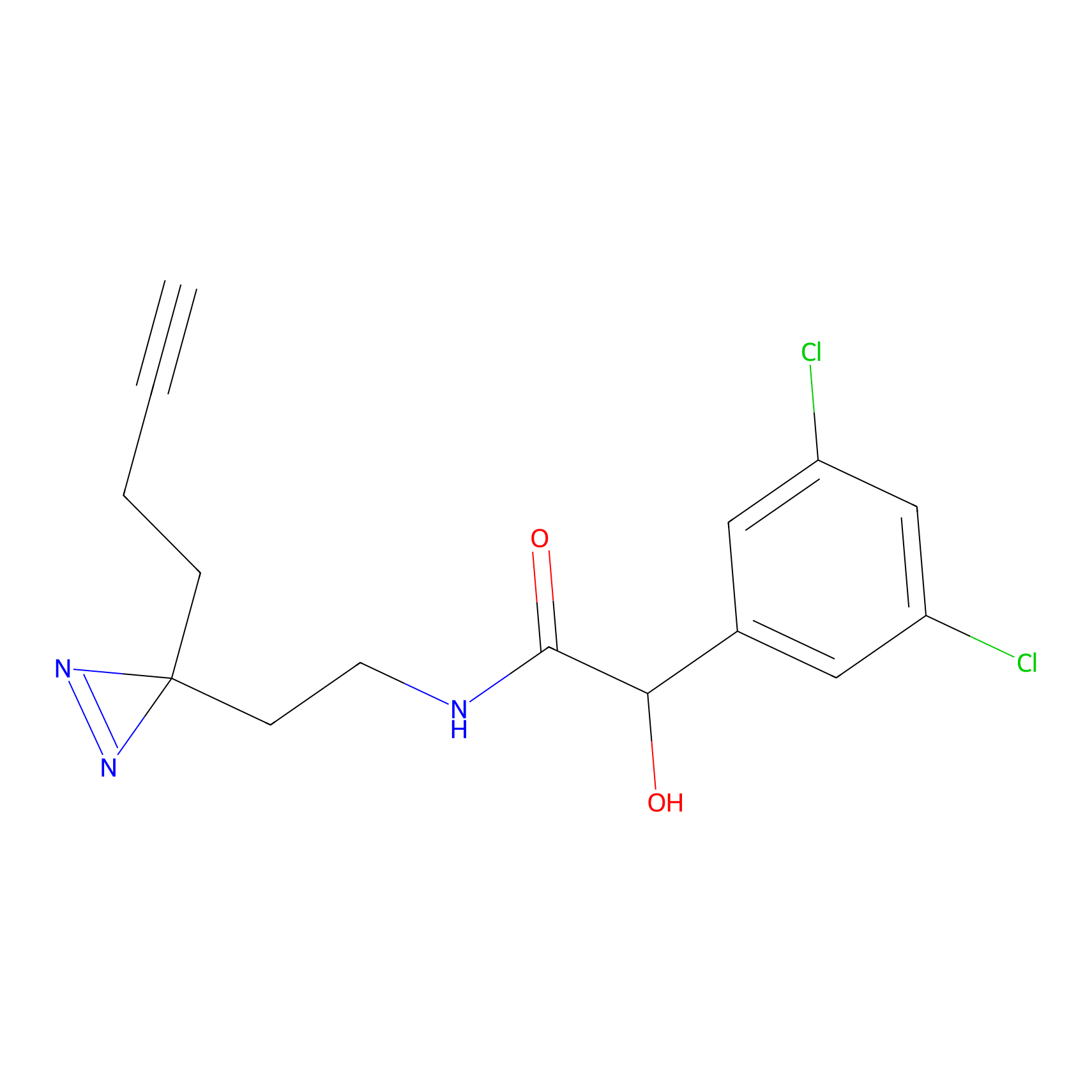
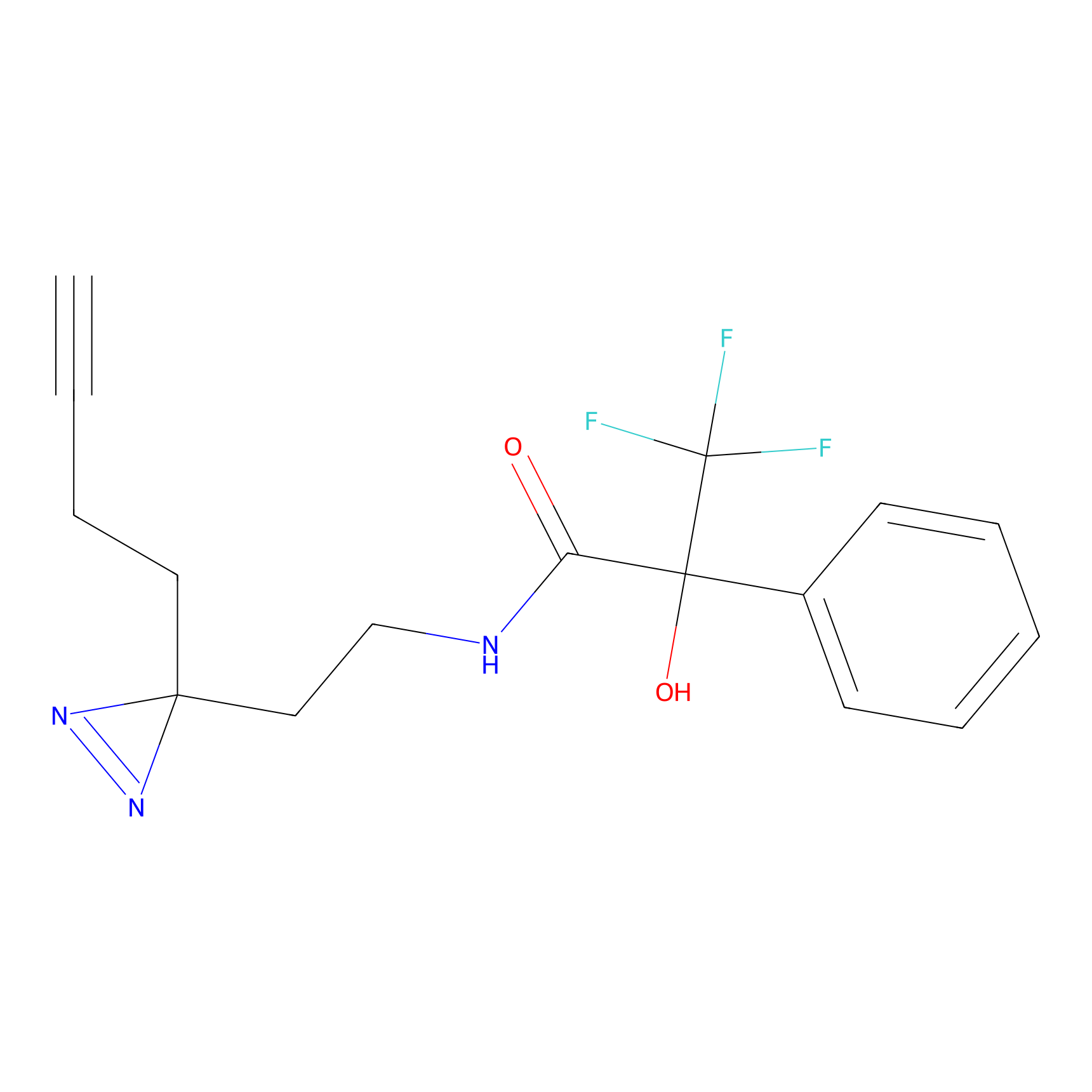
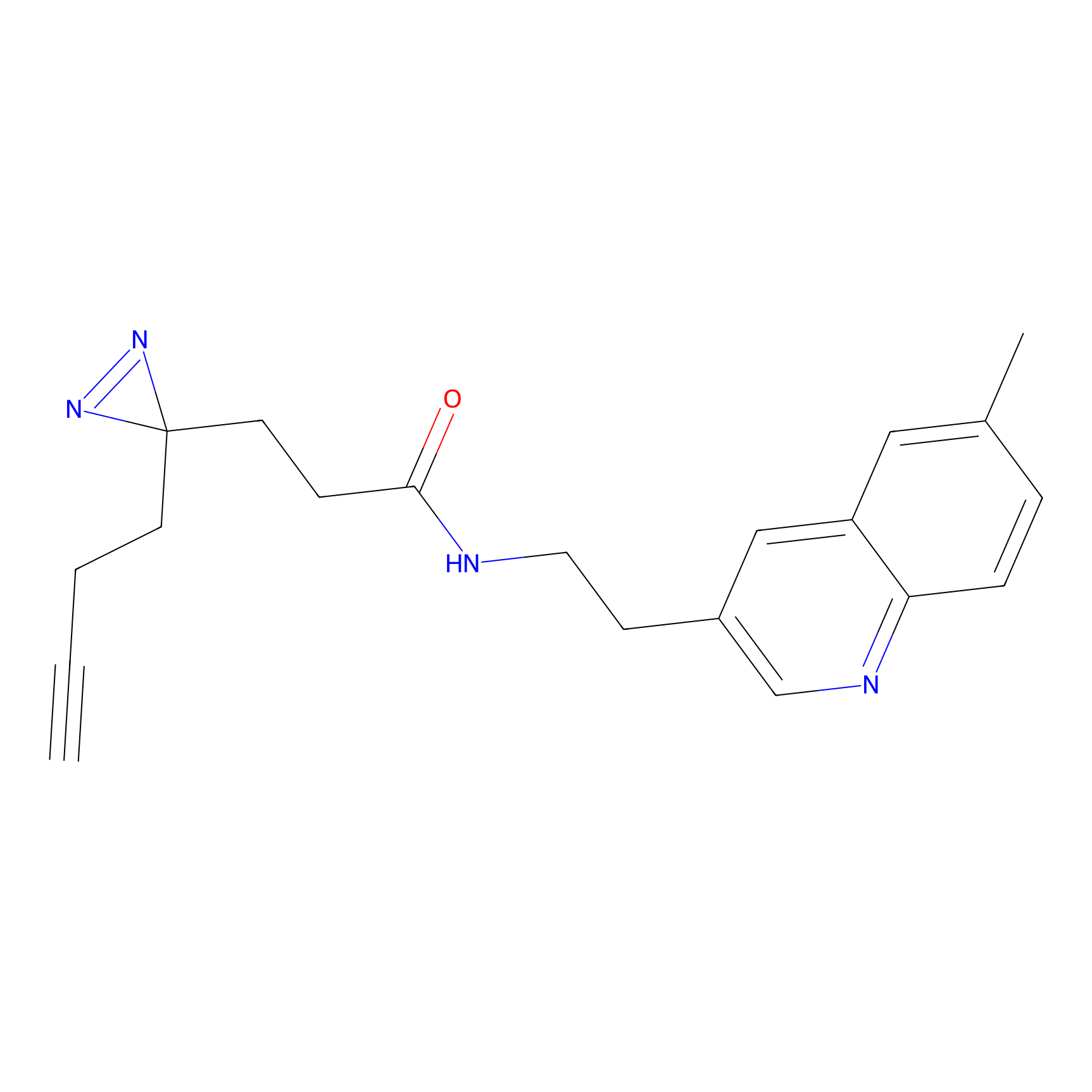
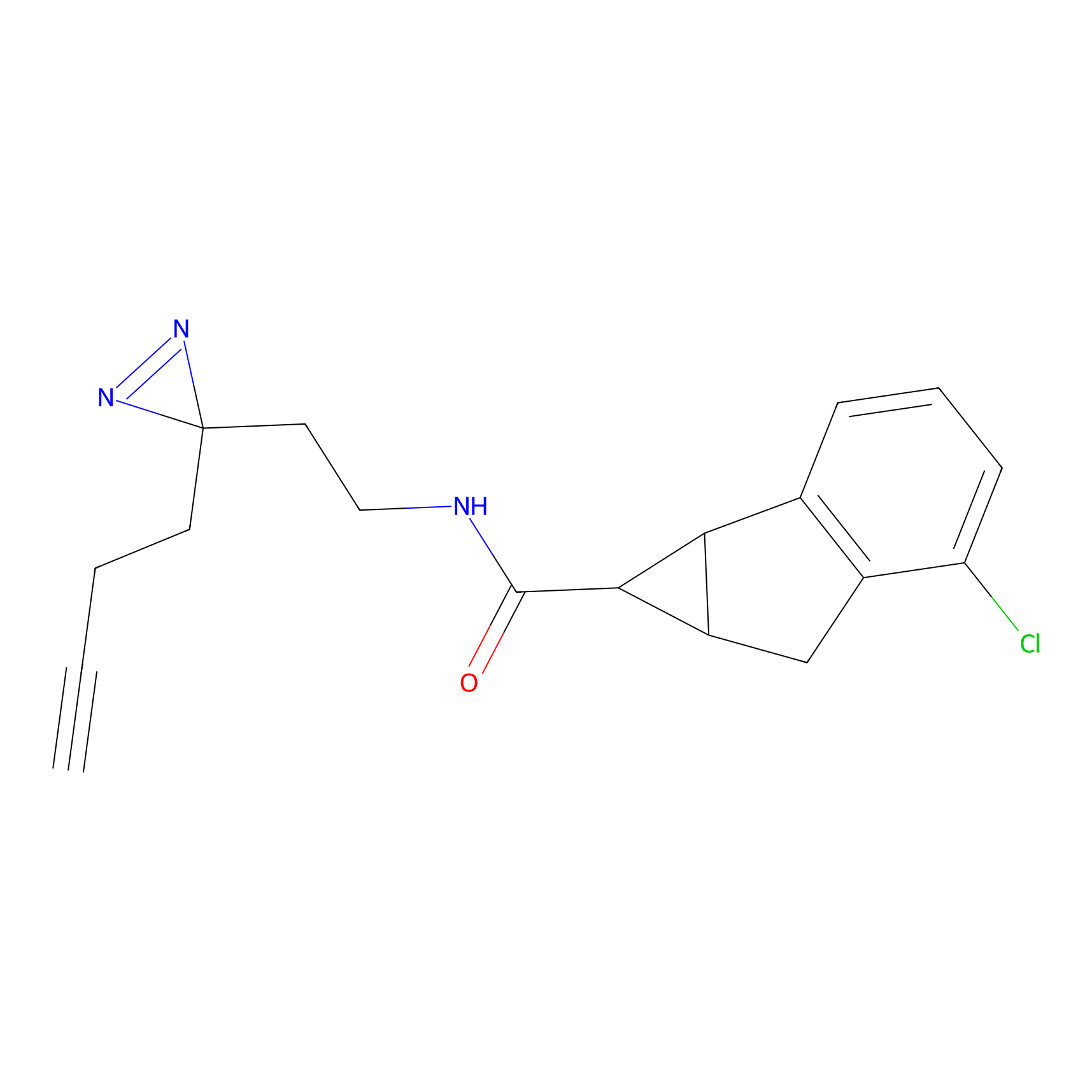
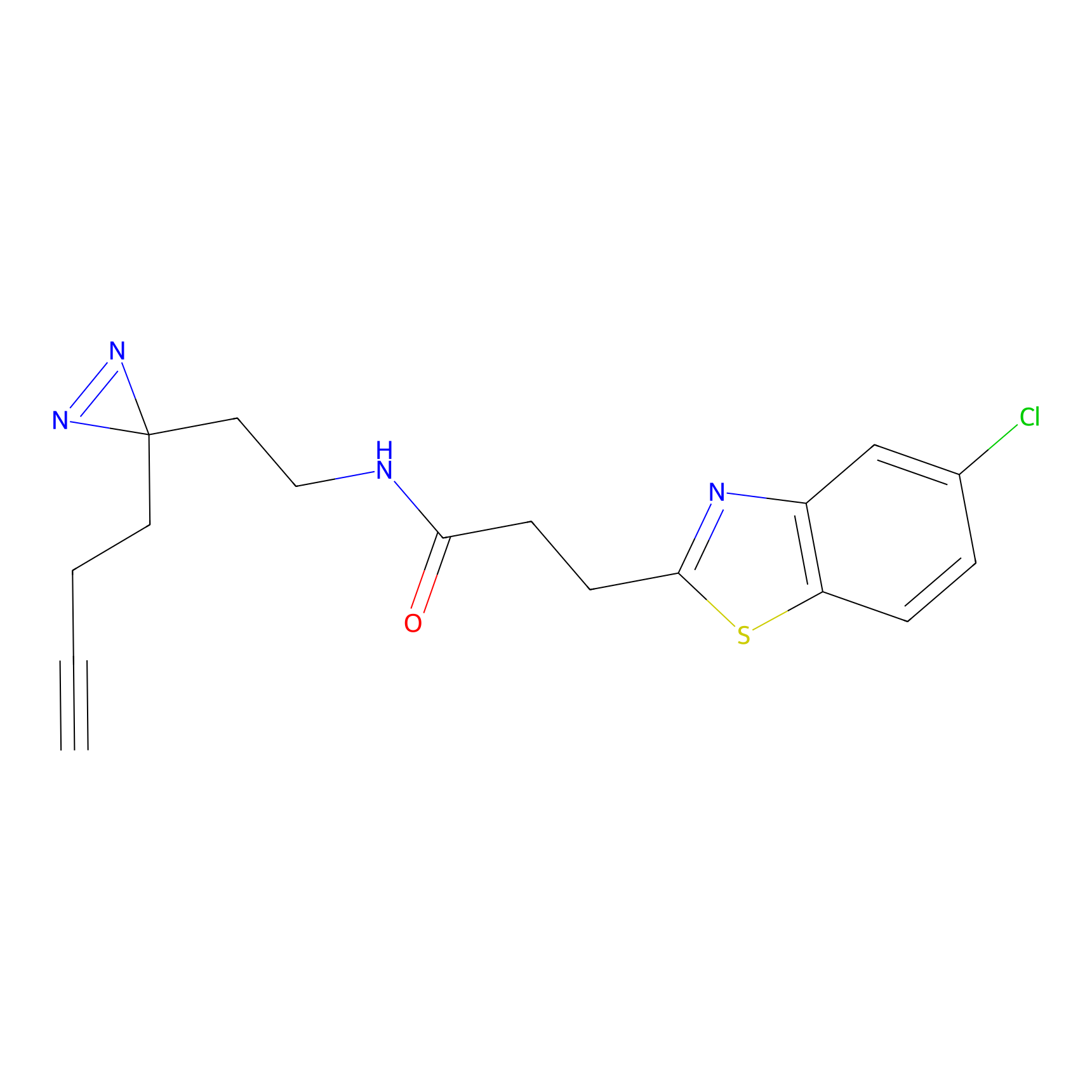
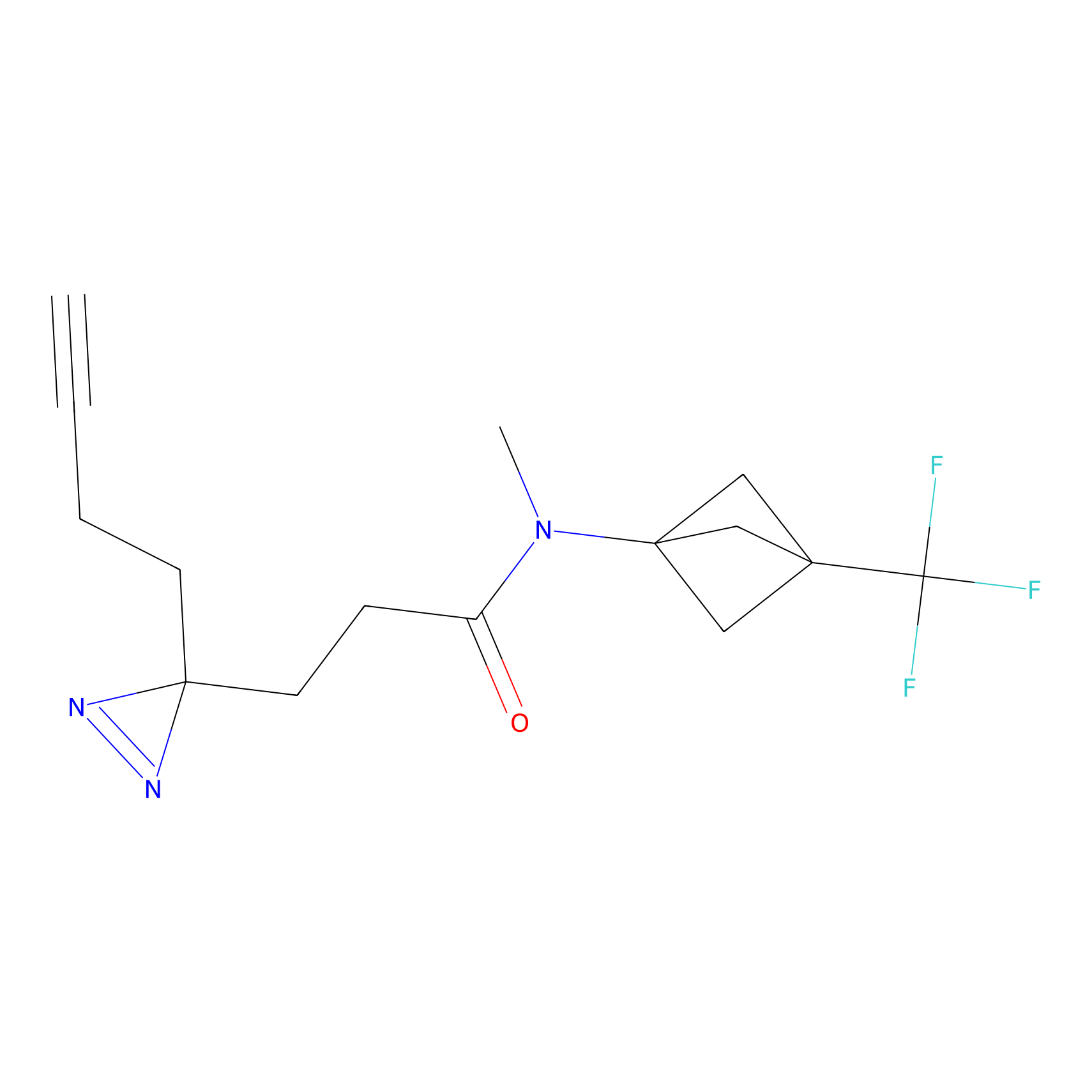
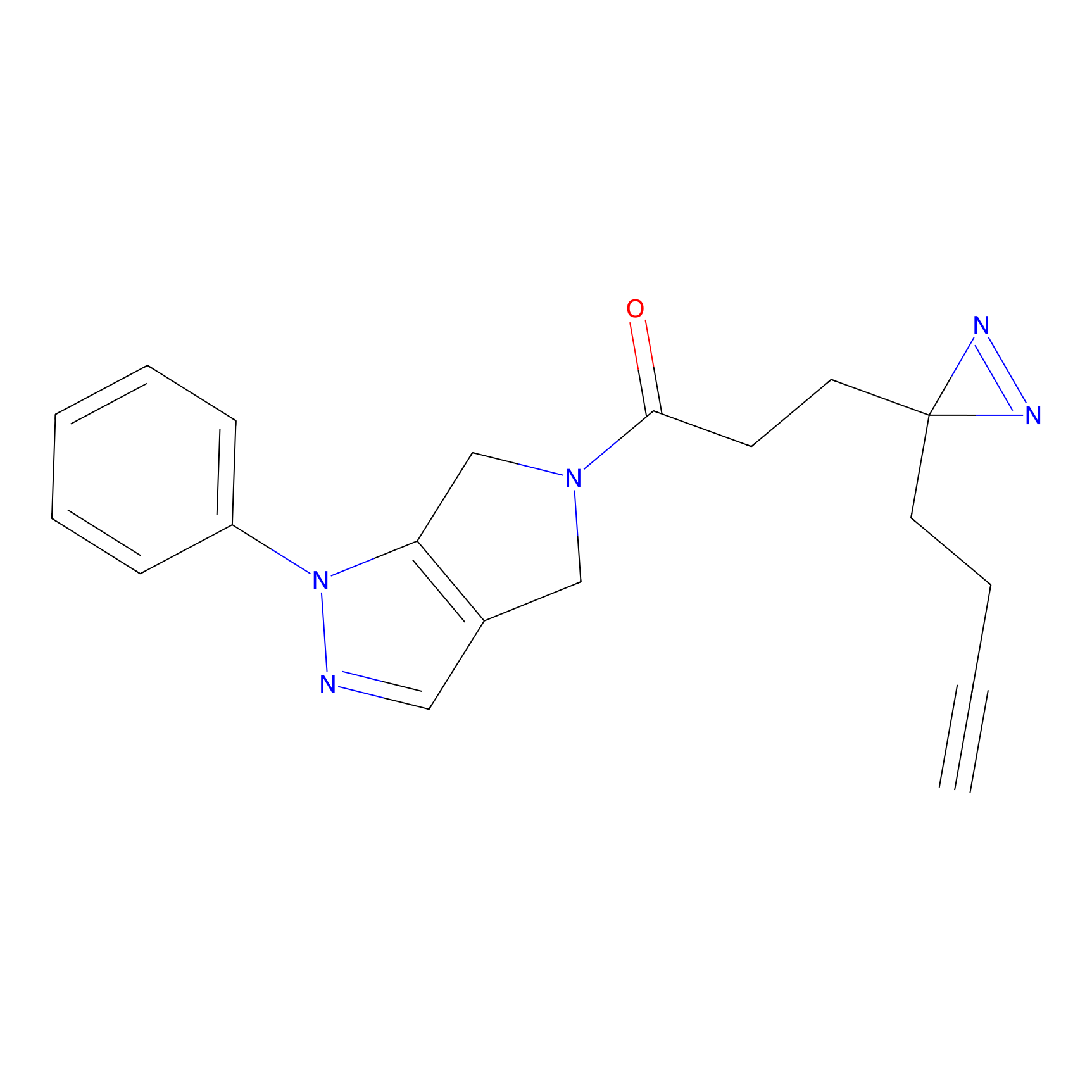
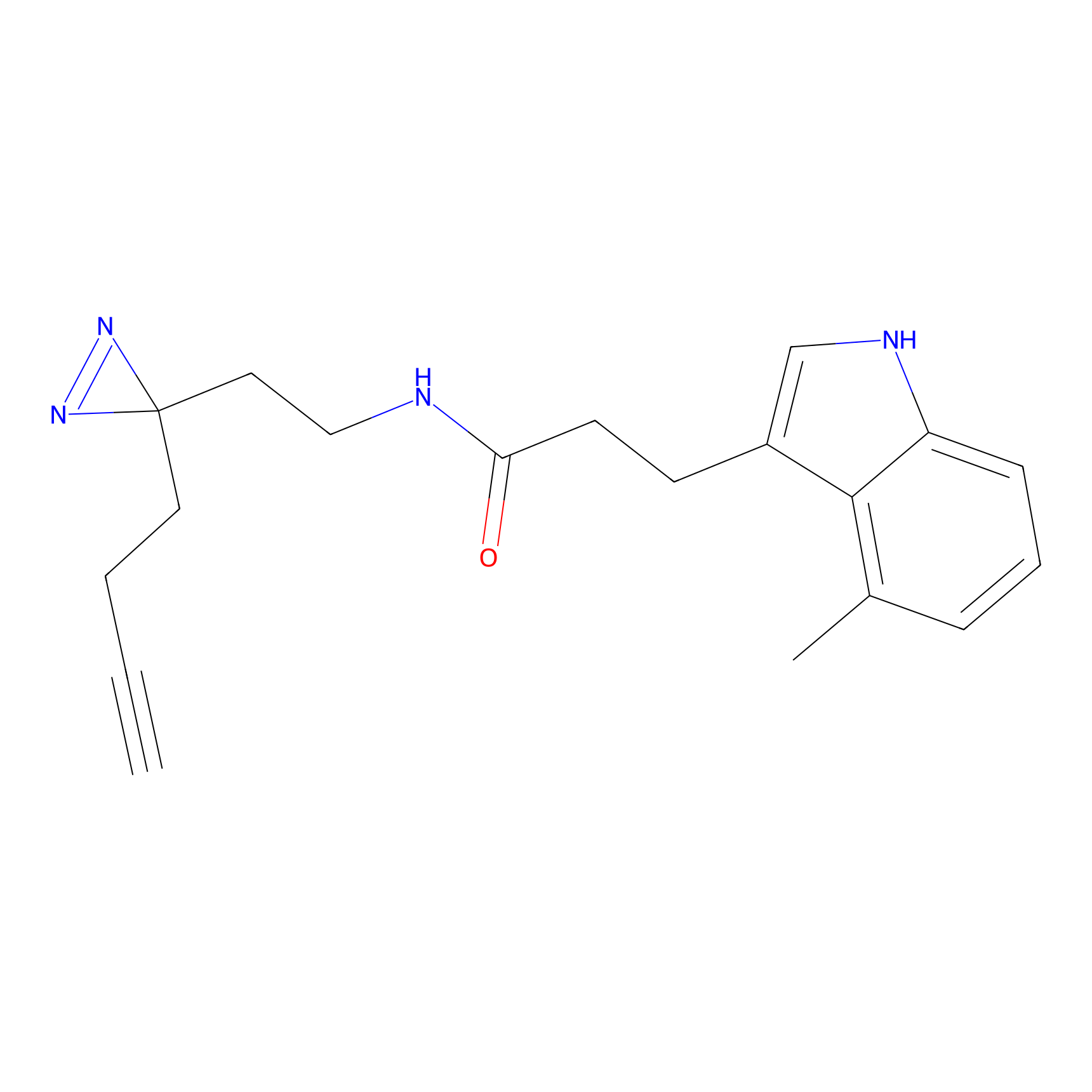
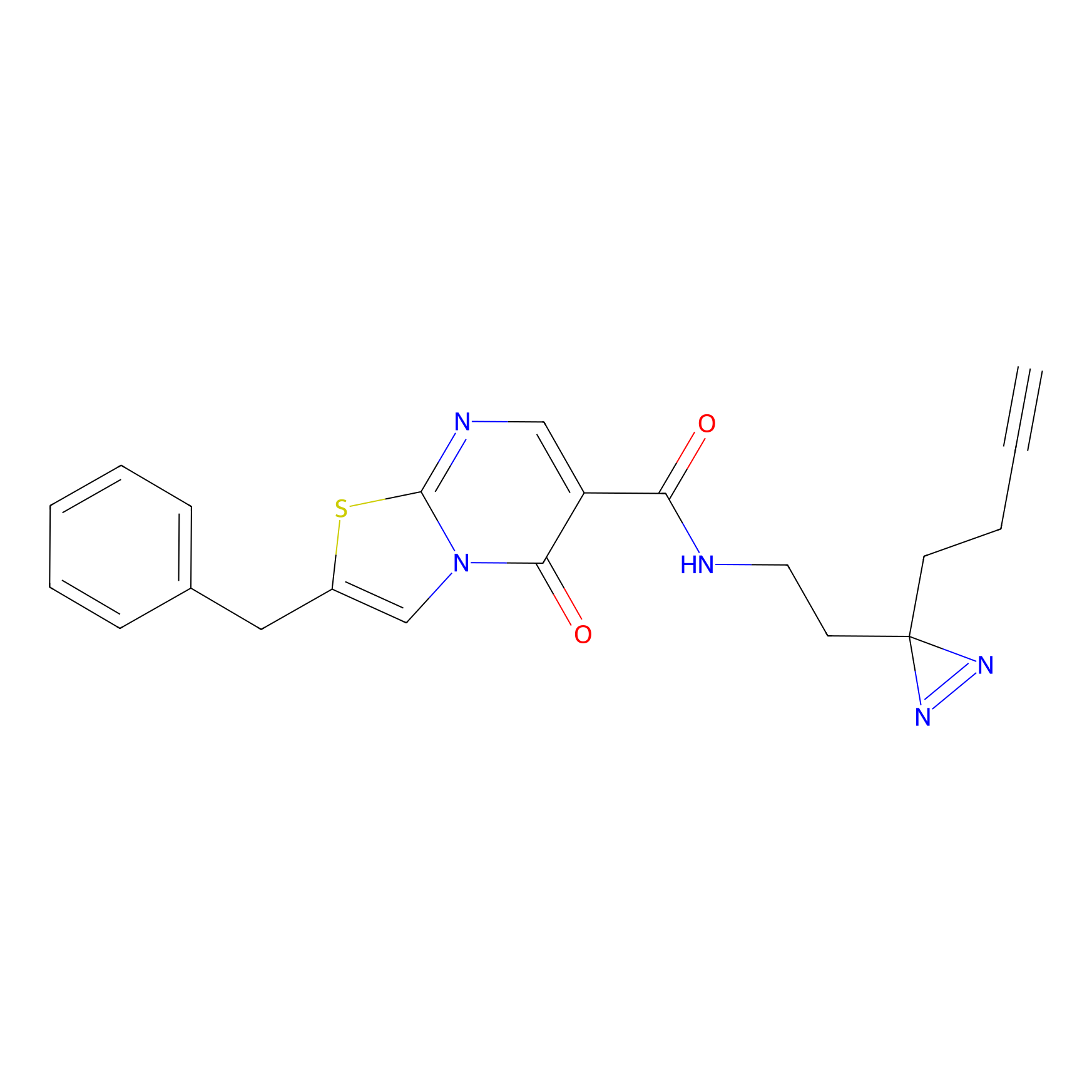
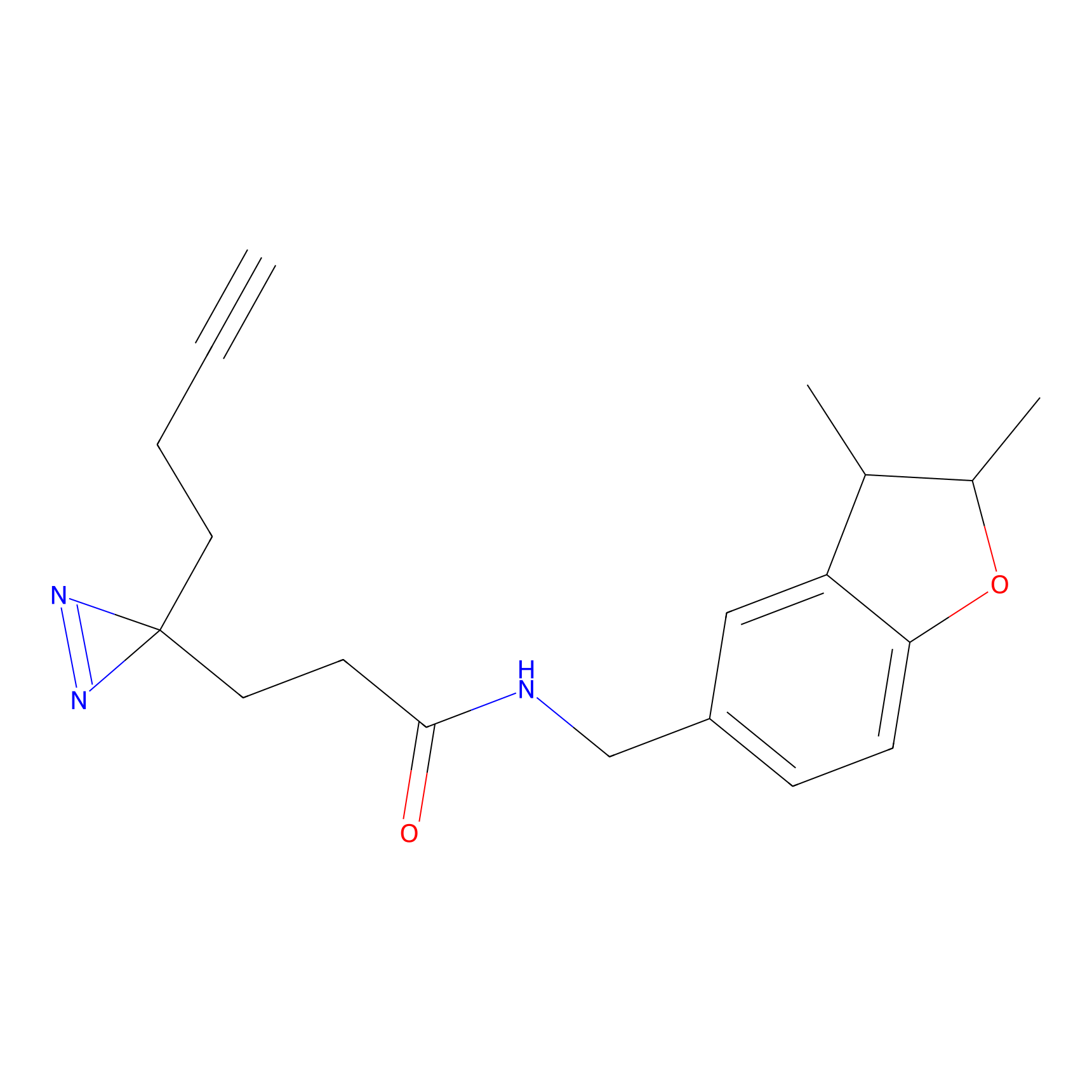
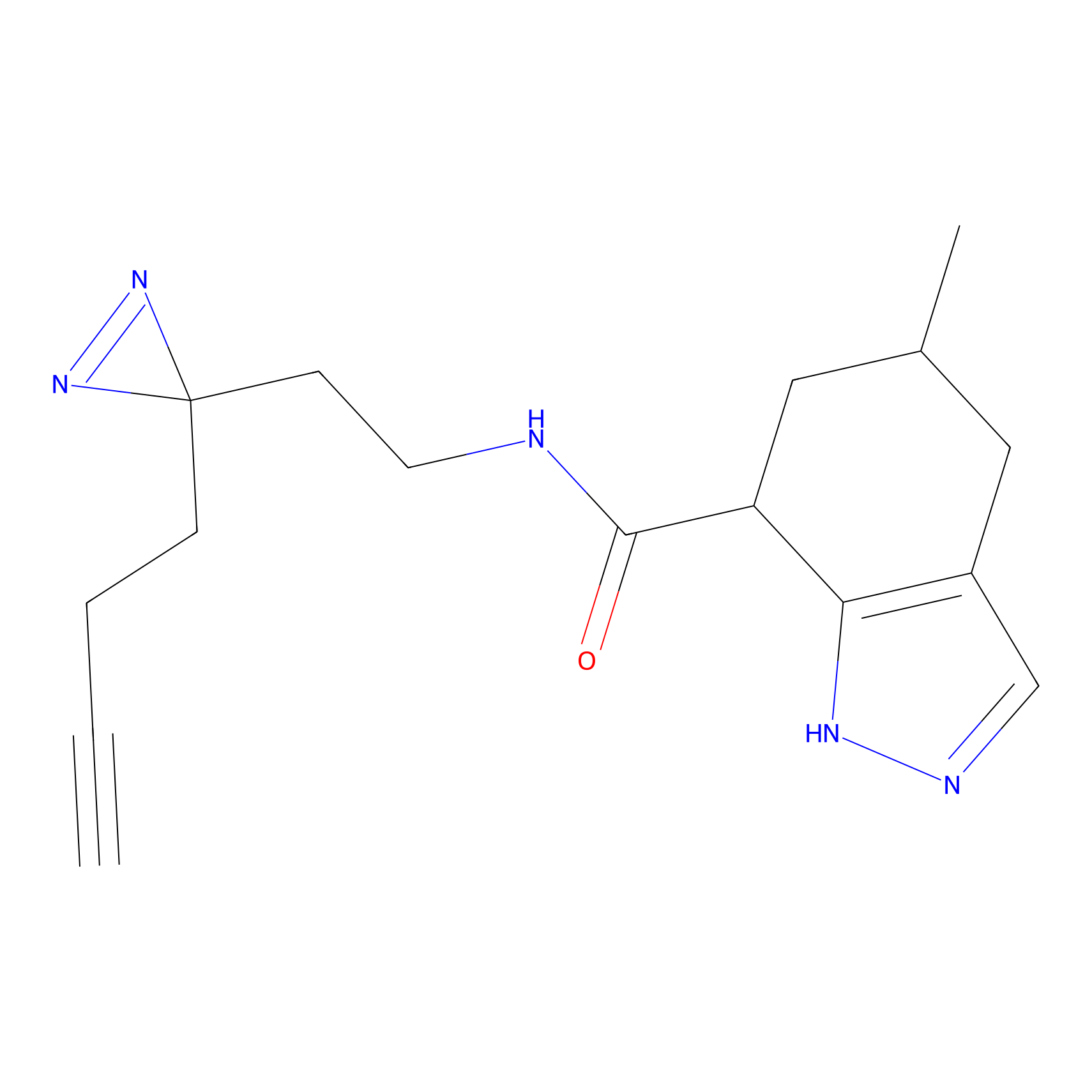
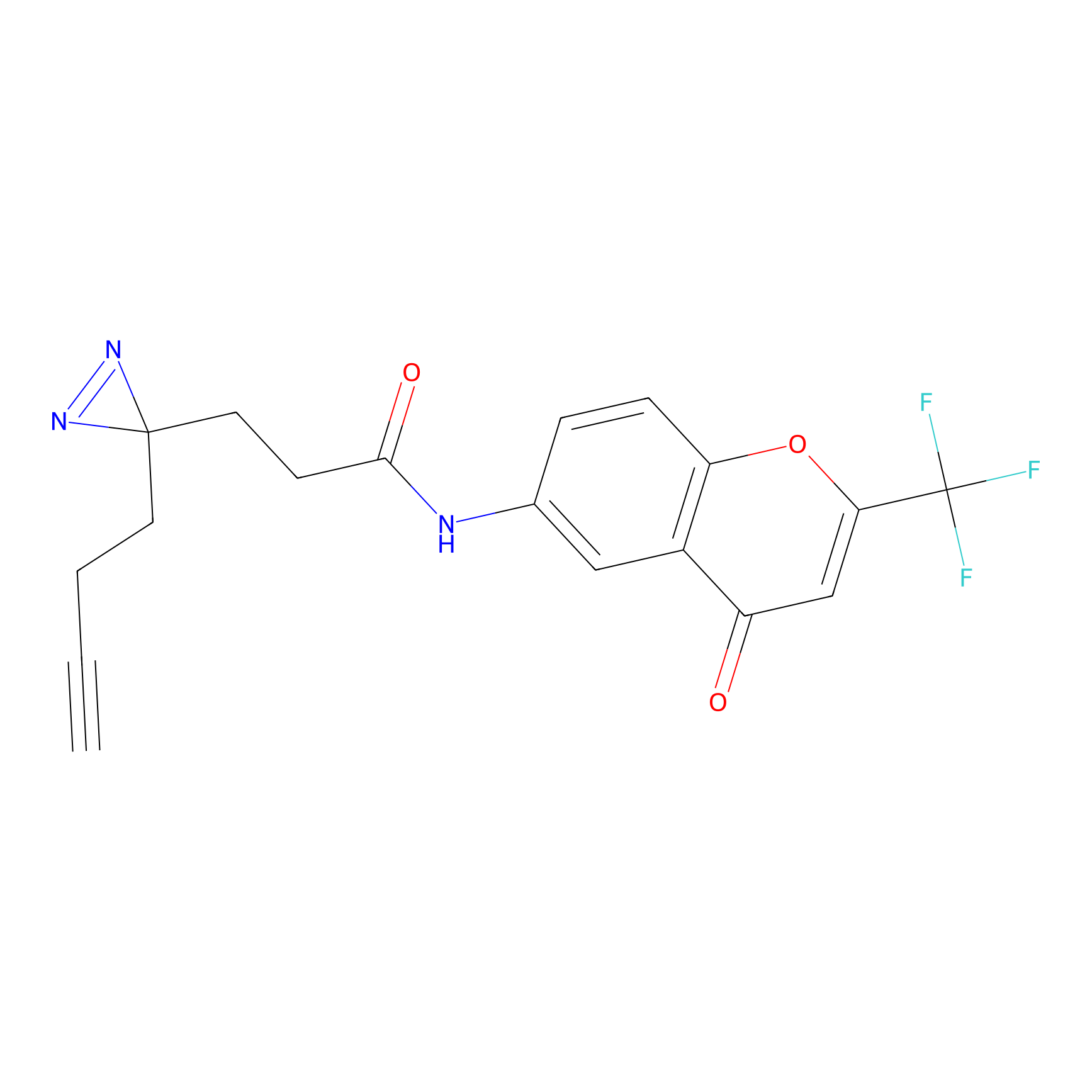
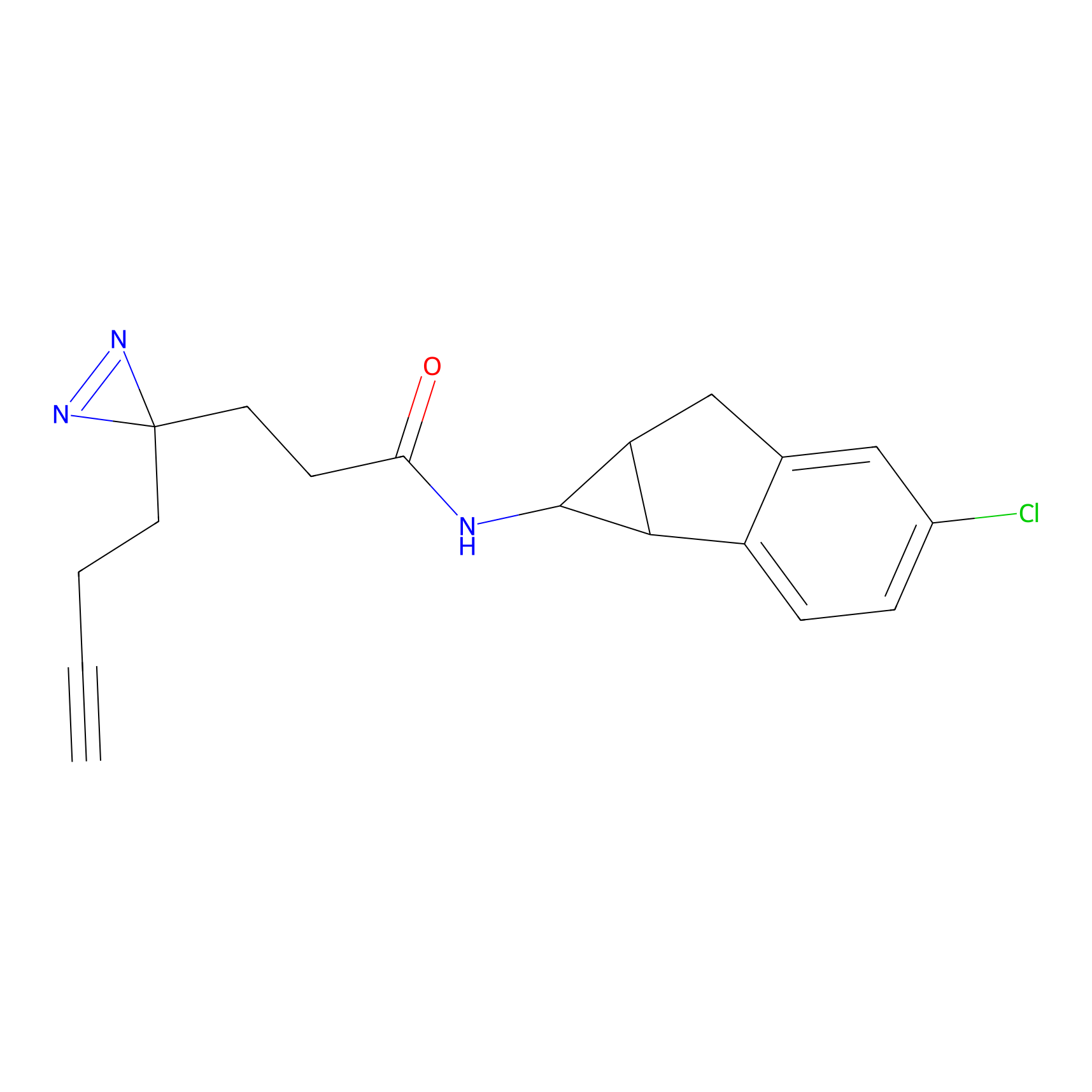
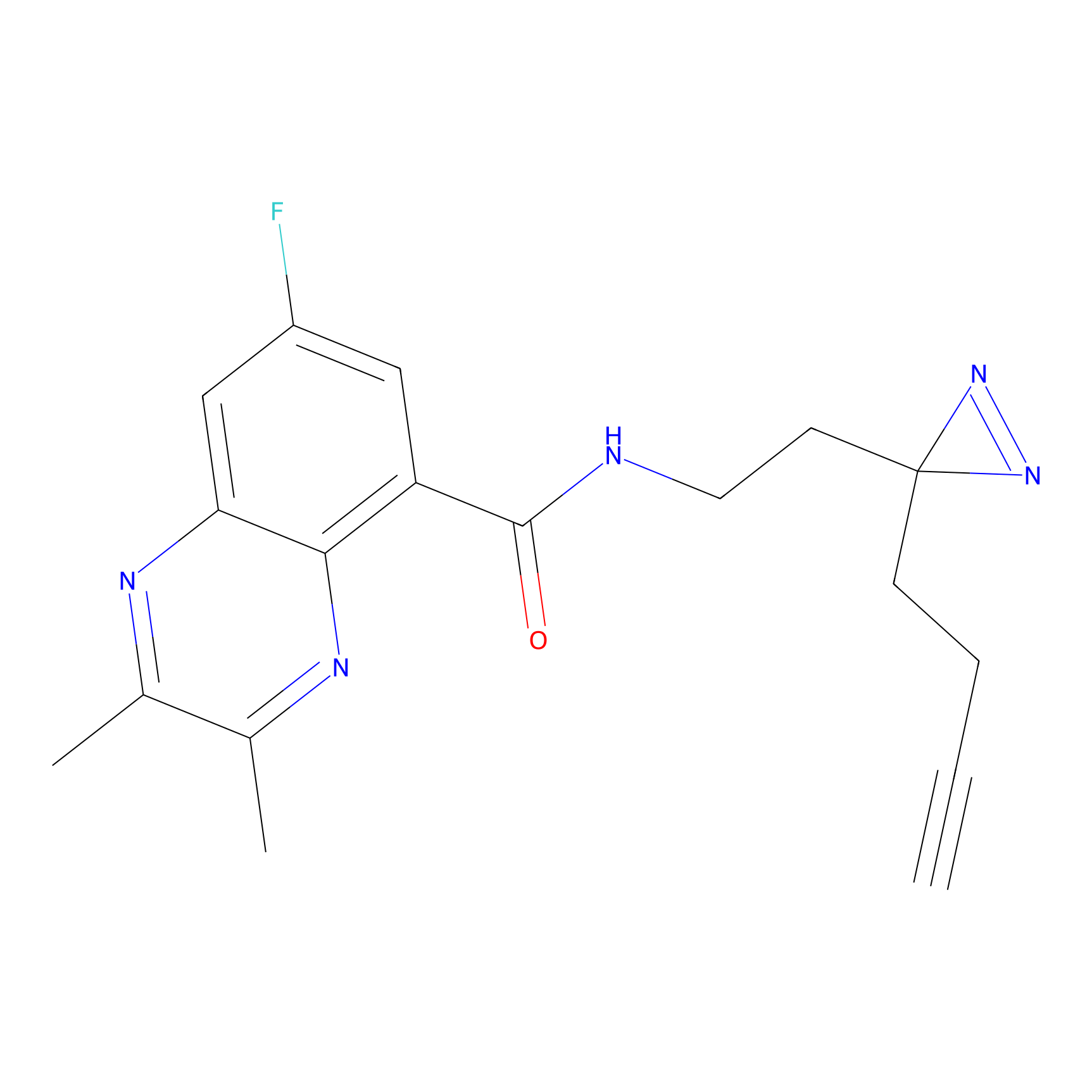
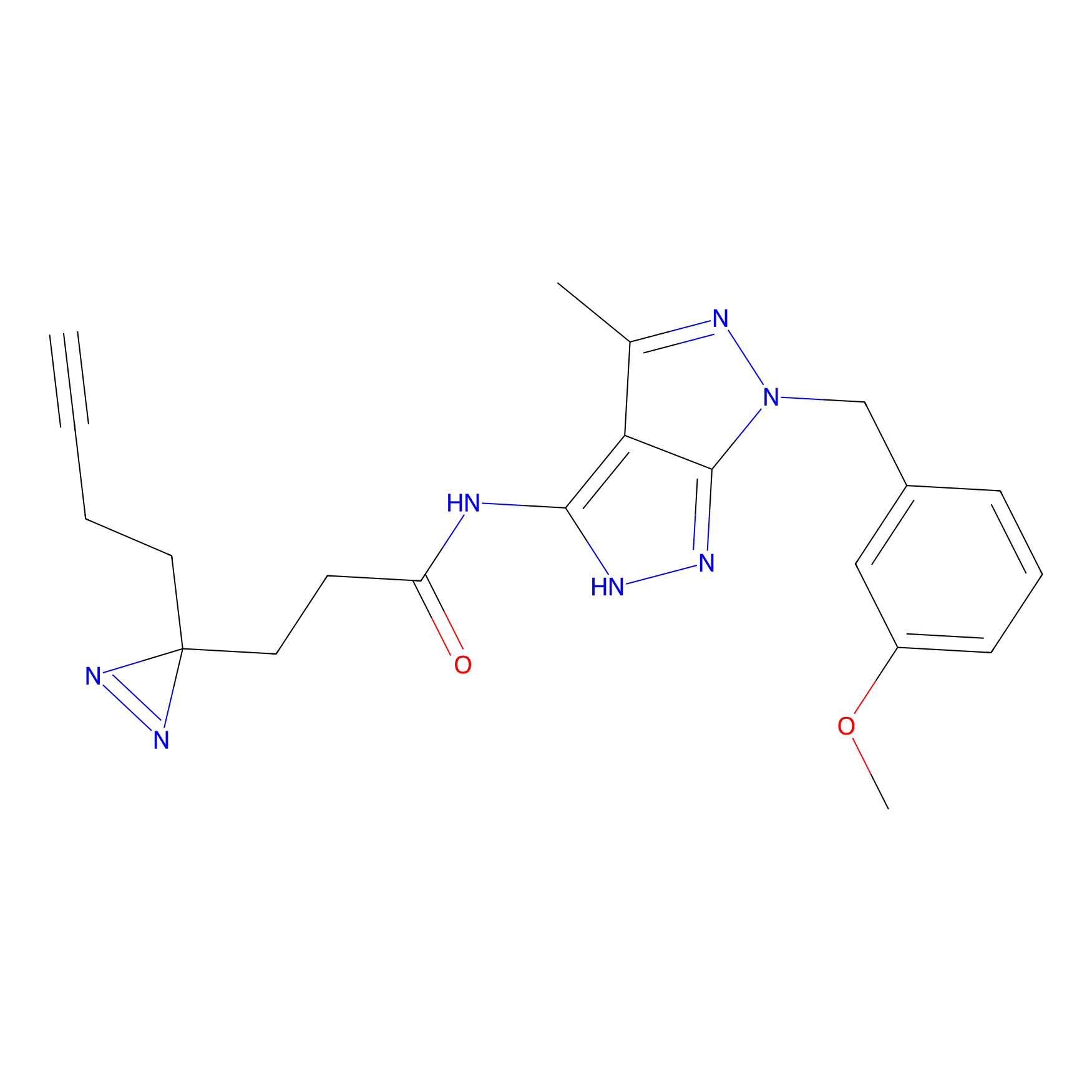
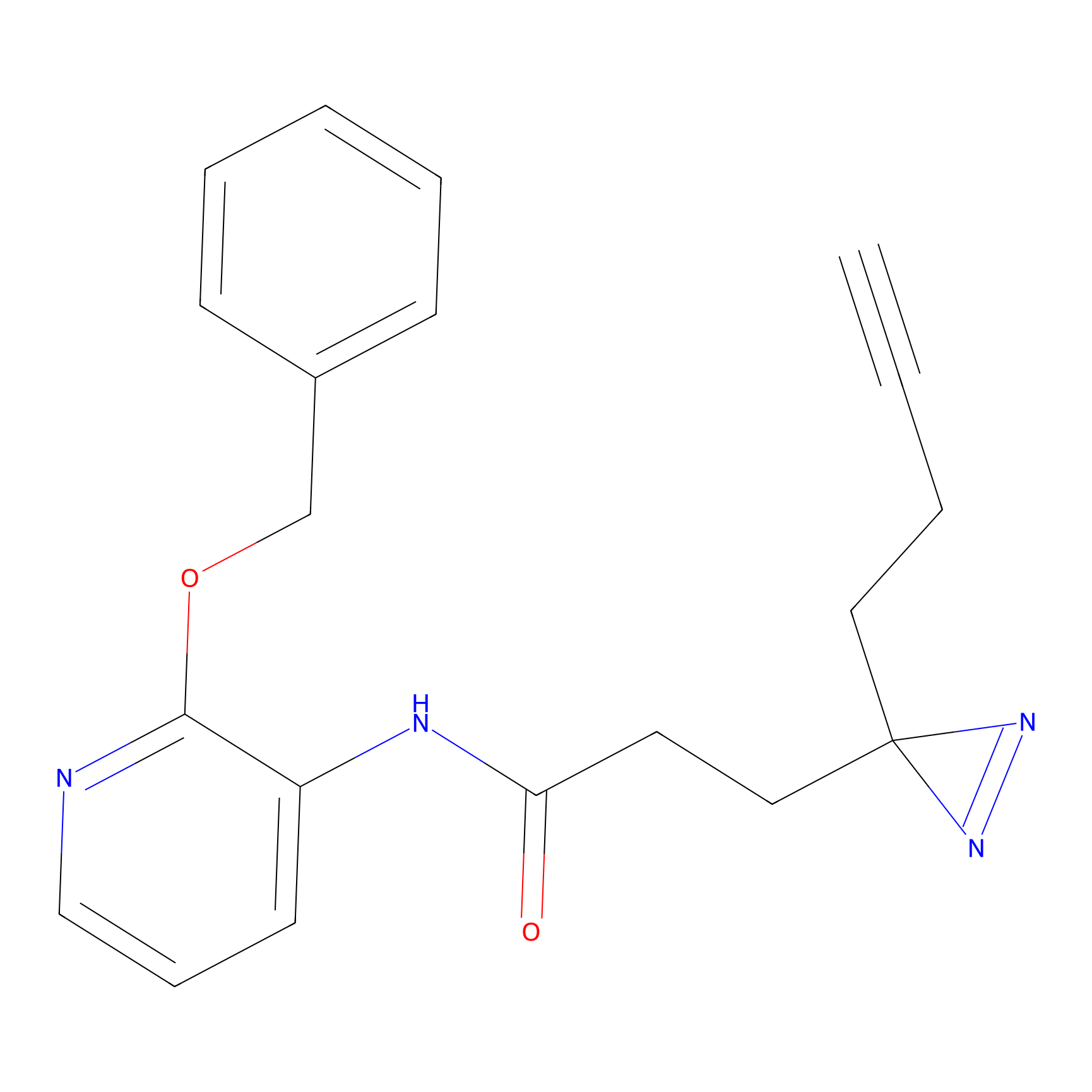
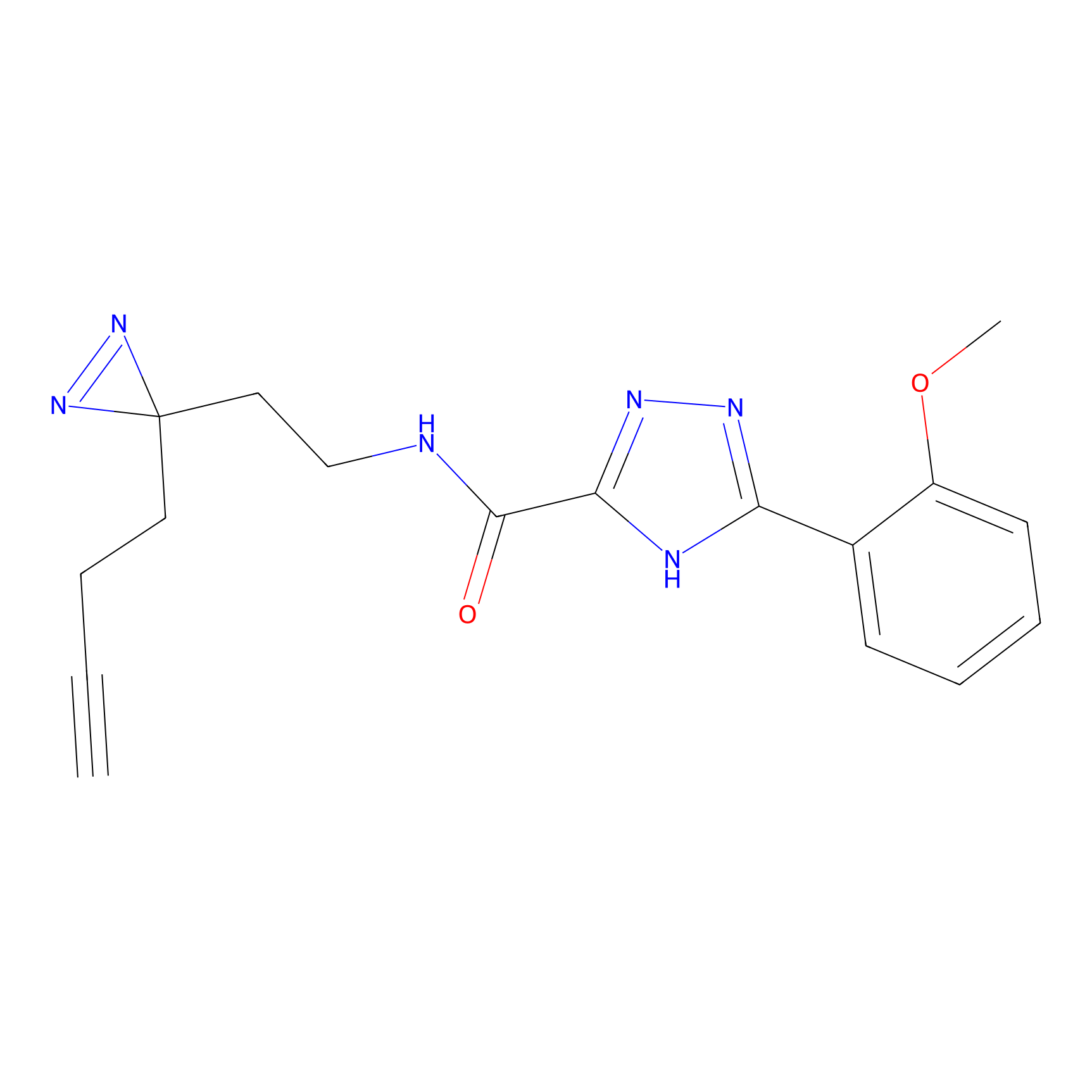
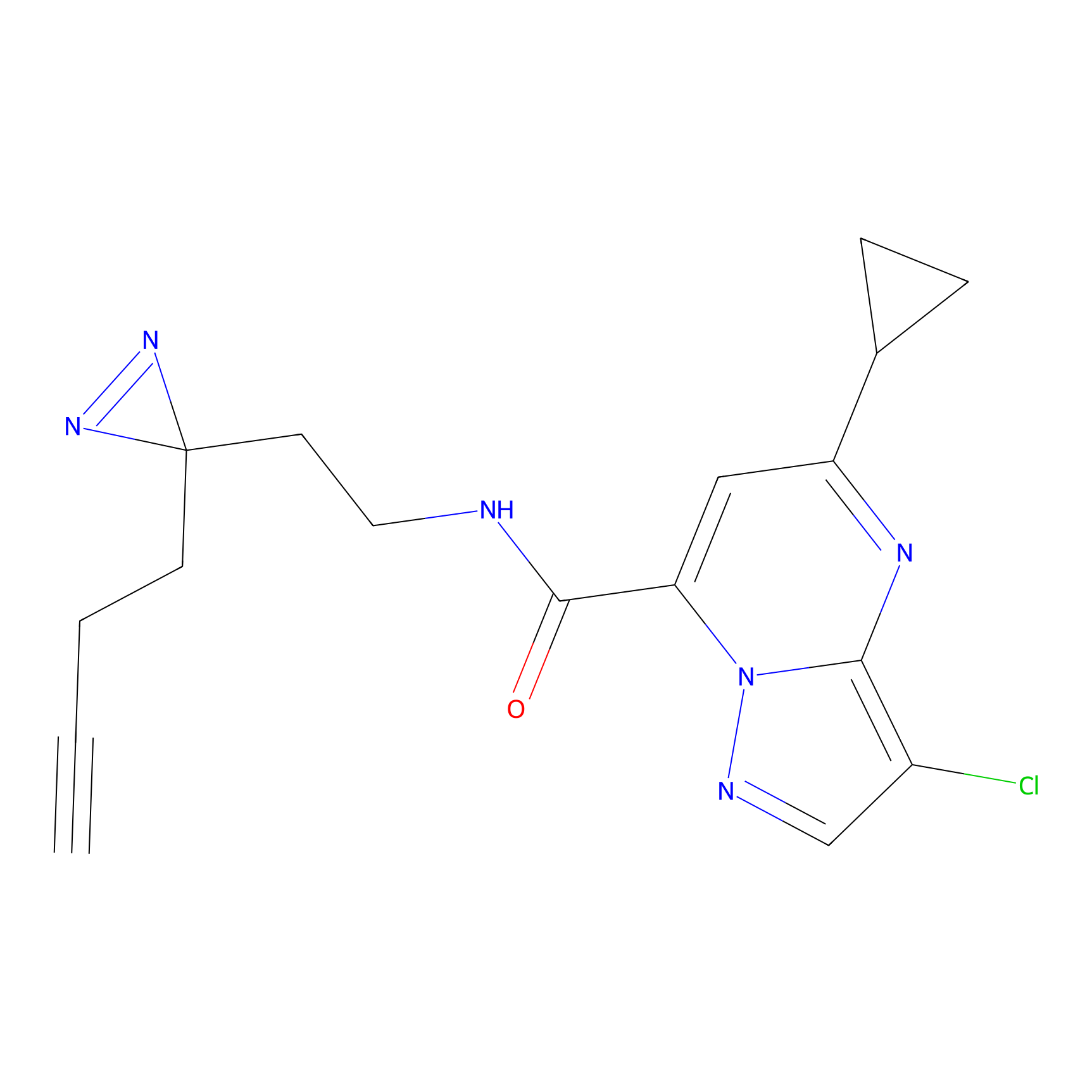
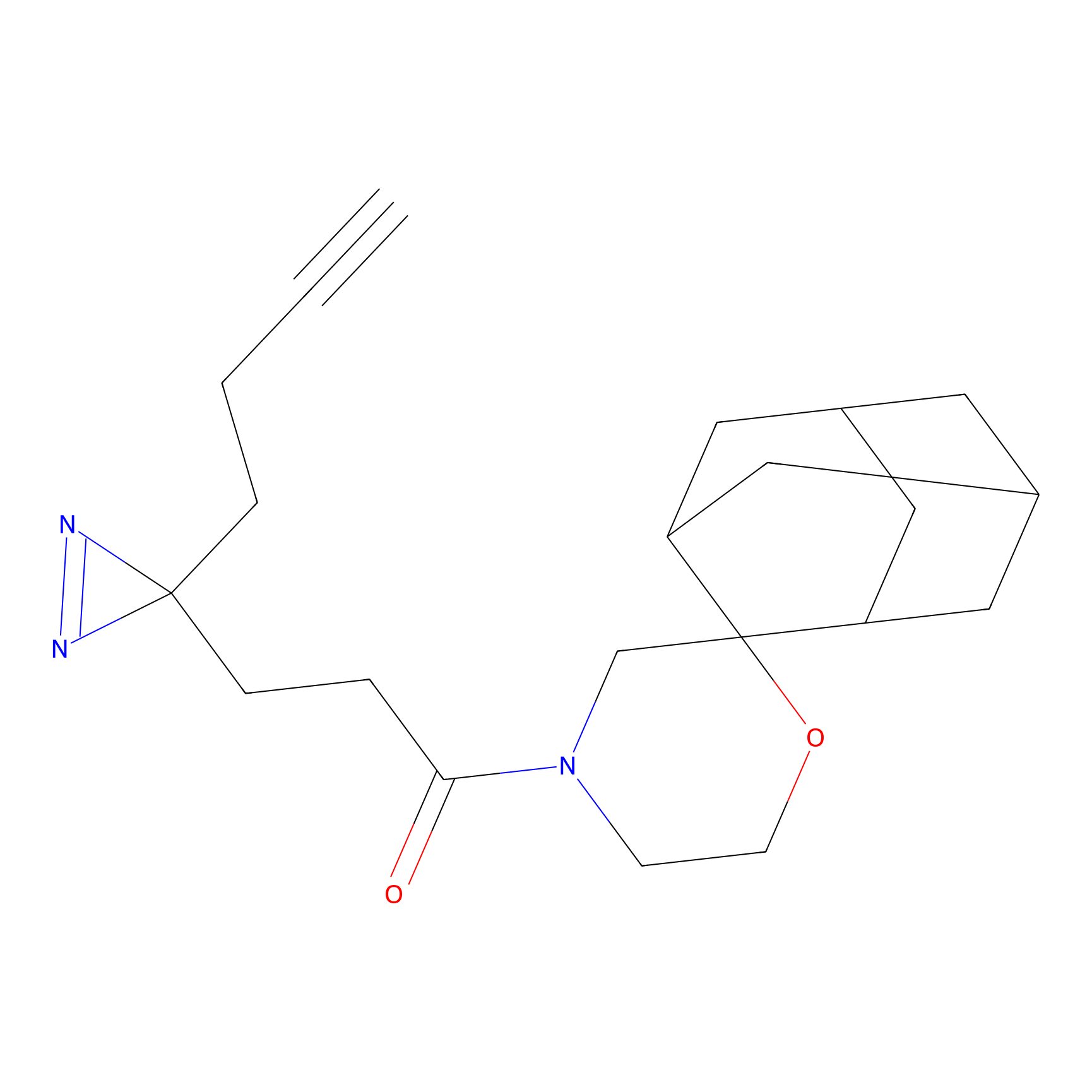
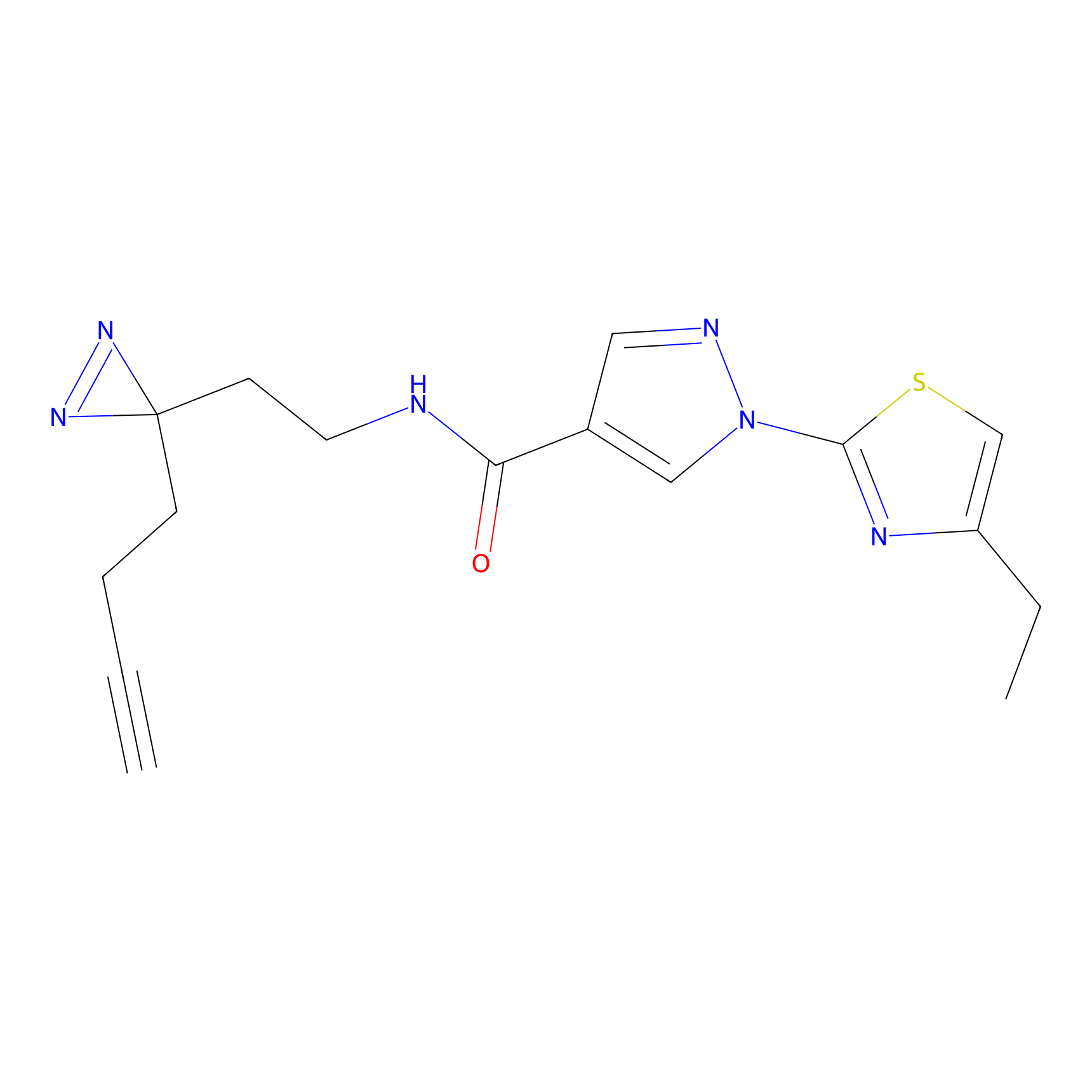
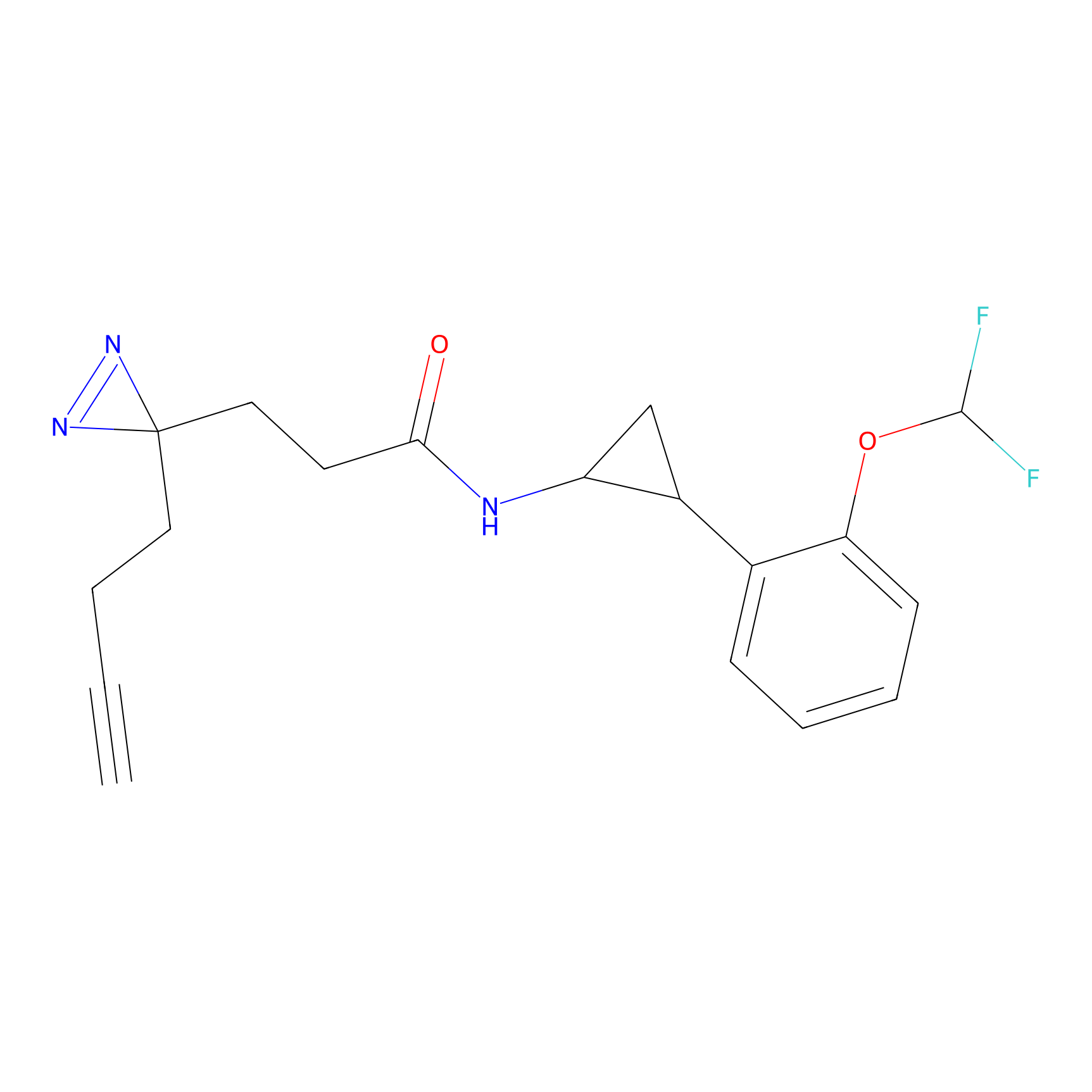
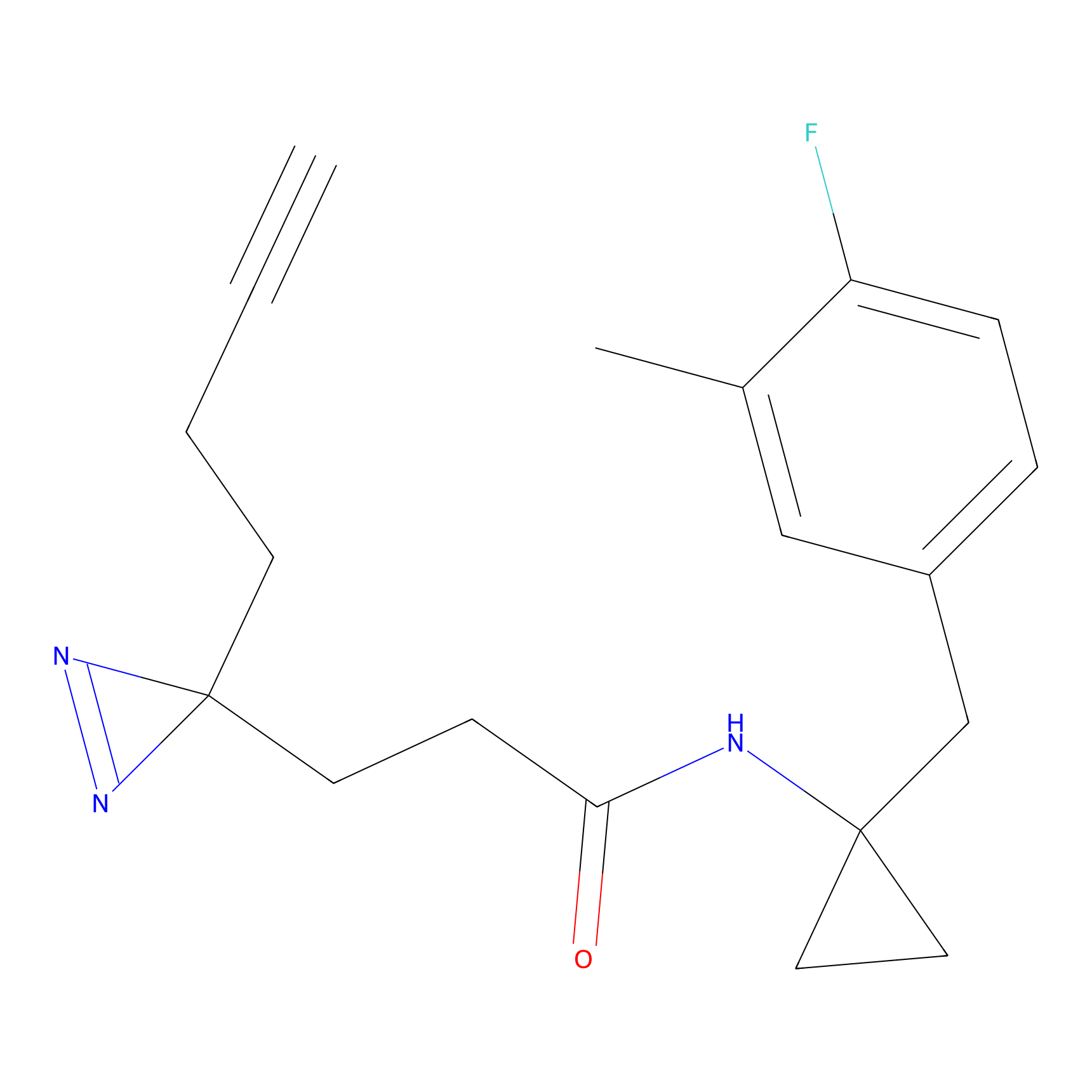
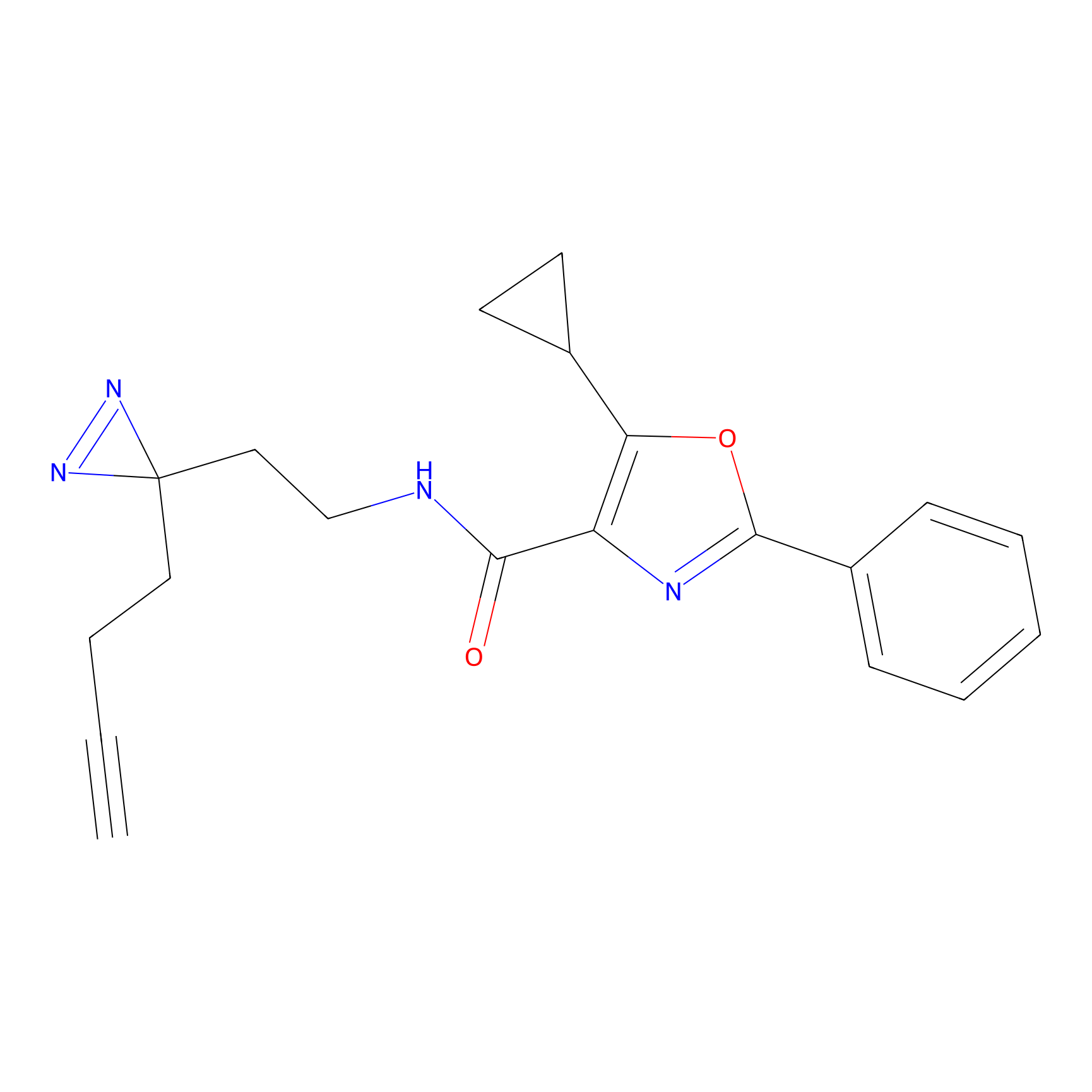
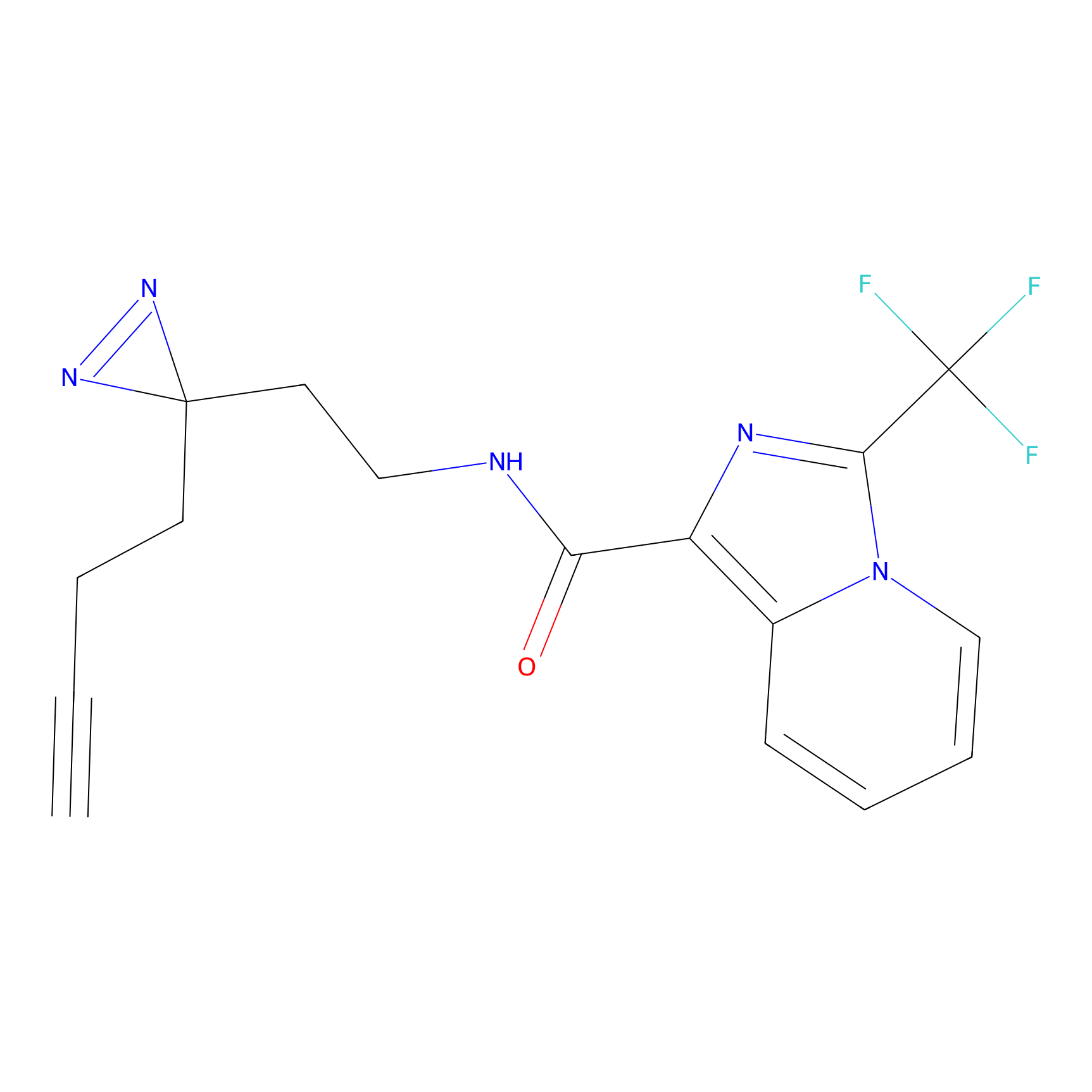
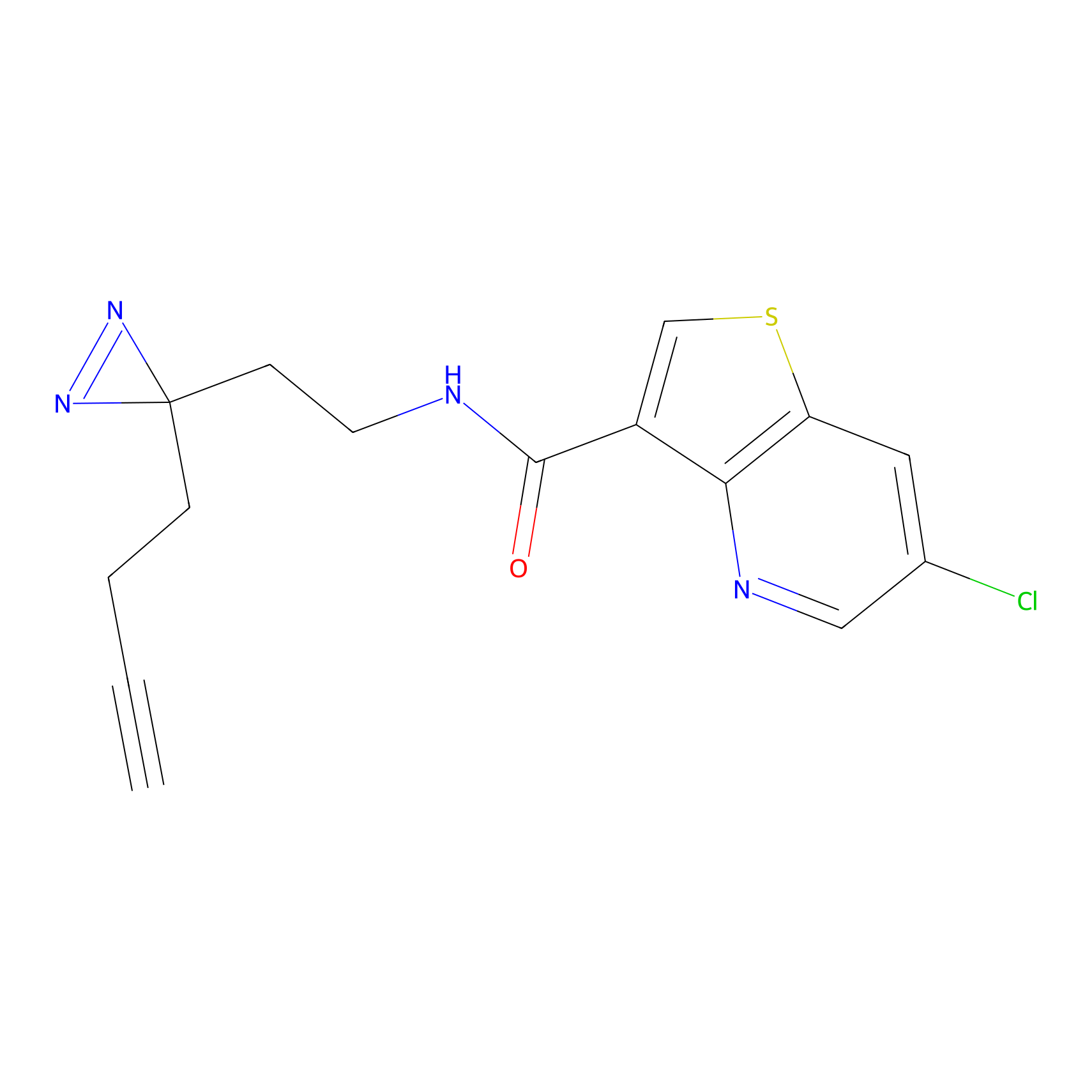
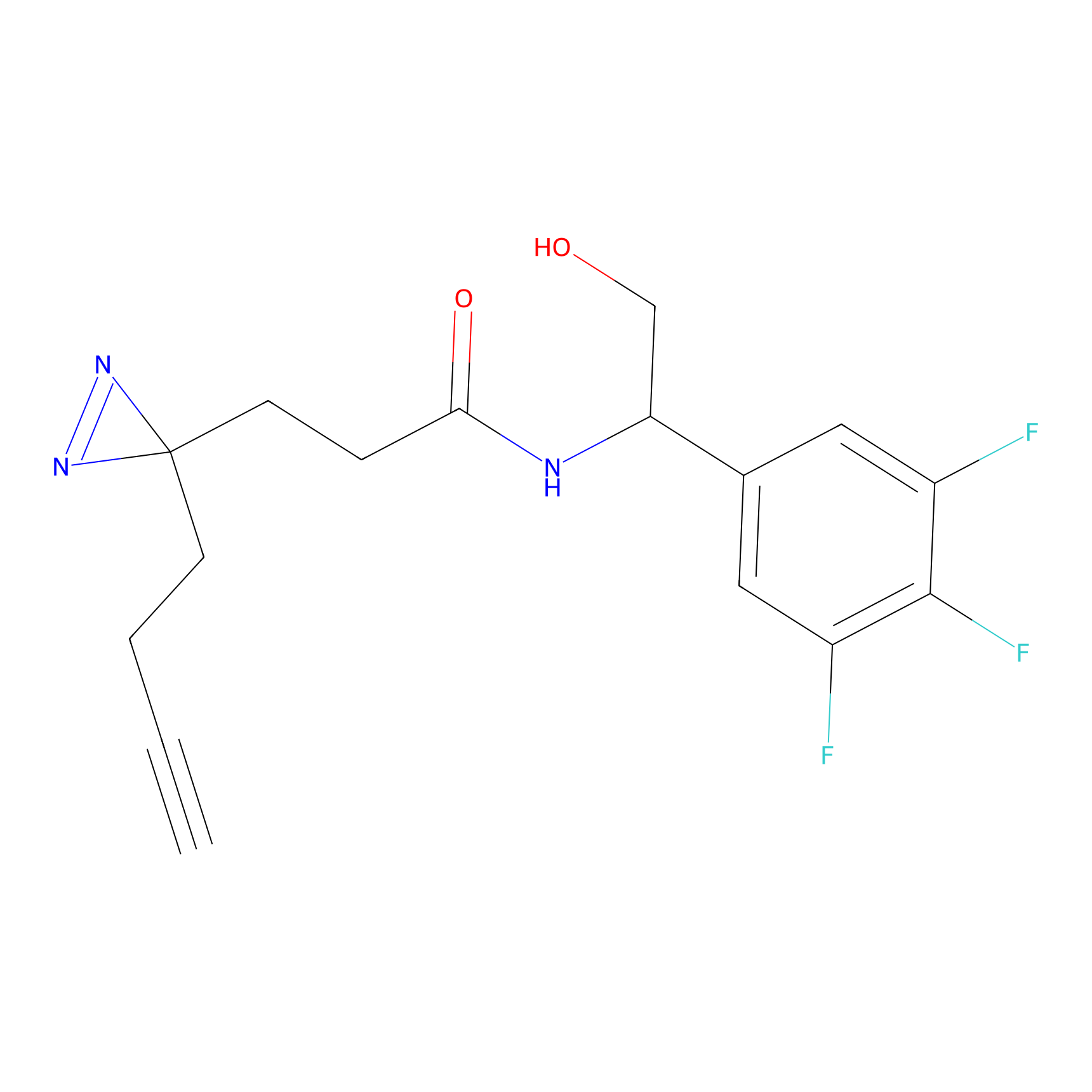
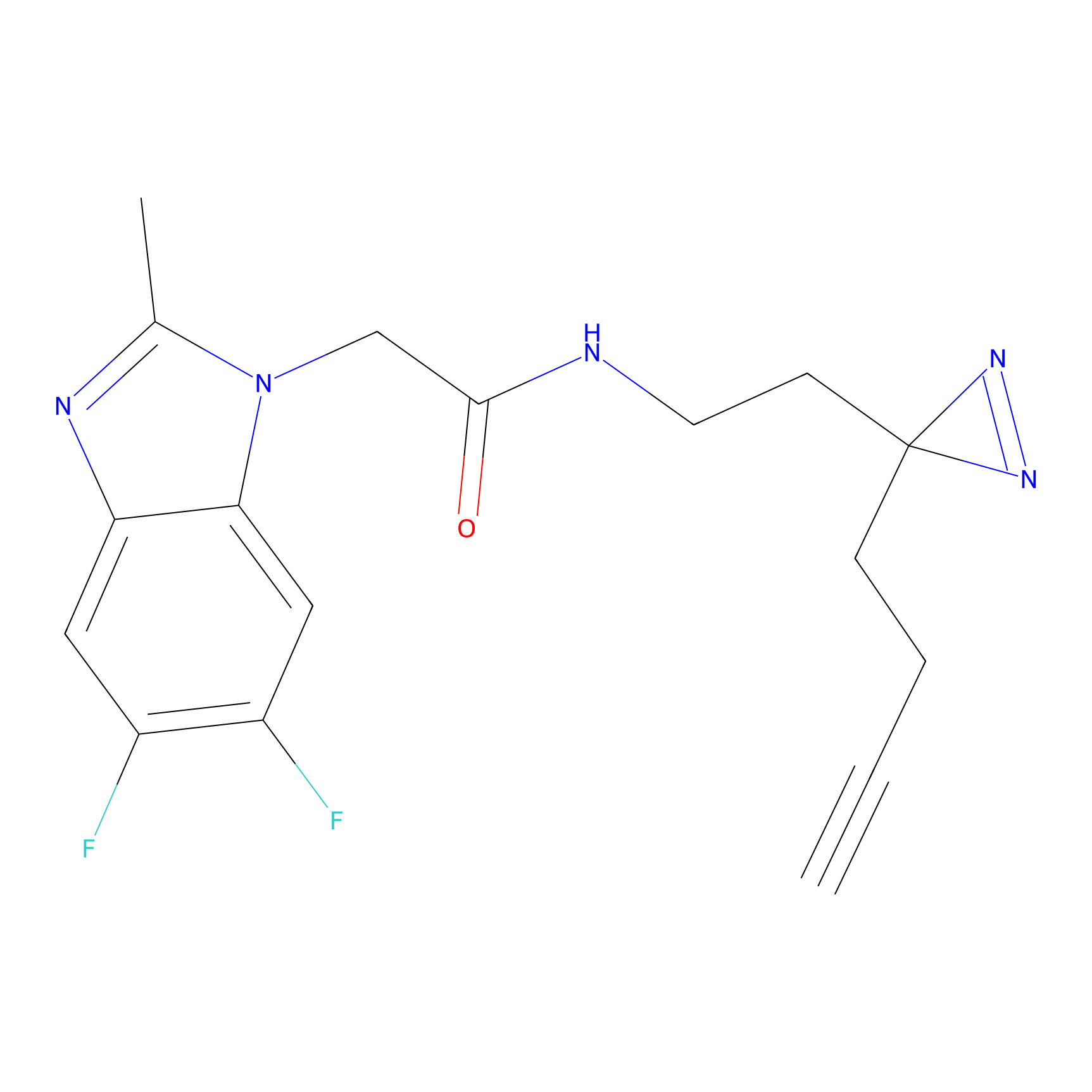
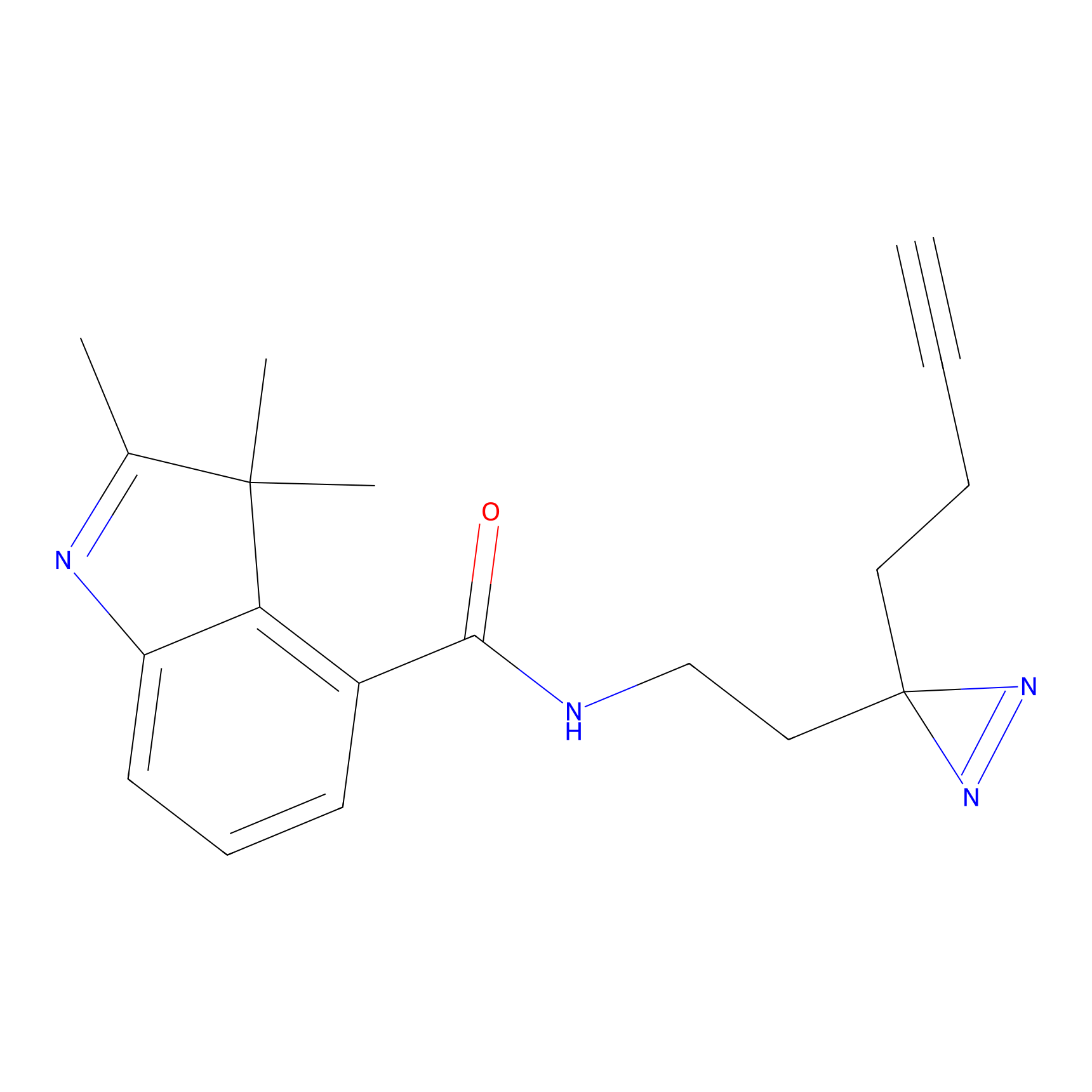
Probe(s) Labeling This Target
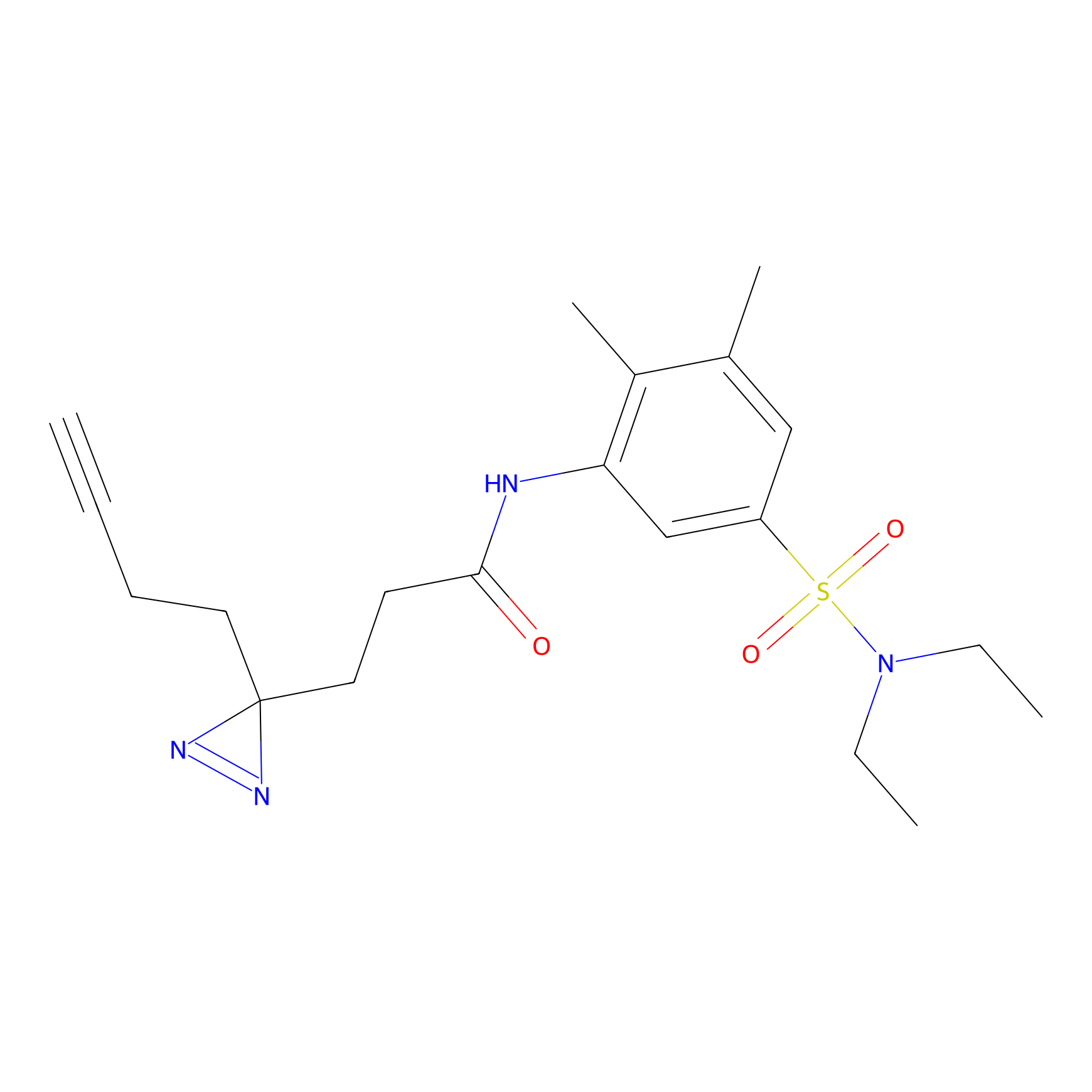
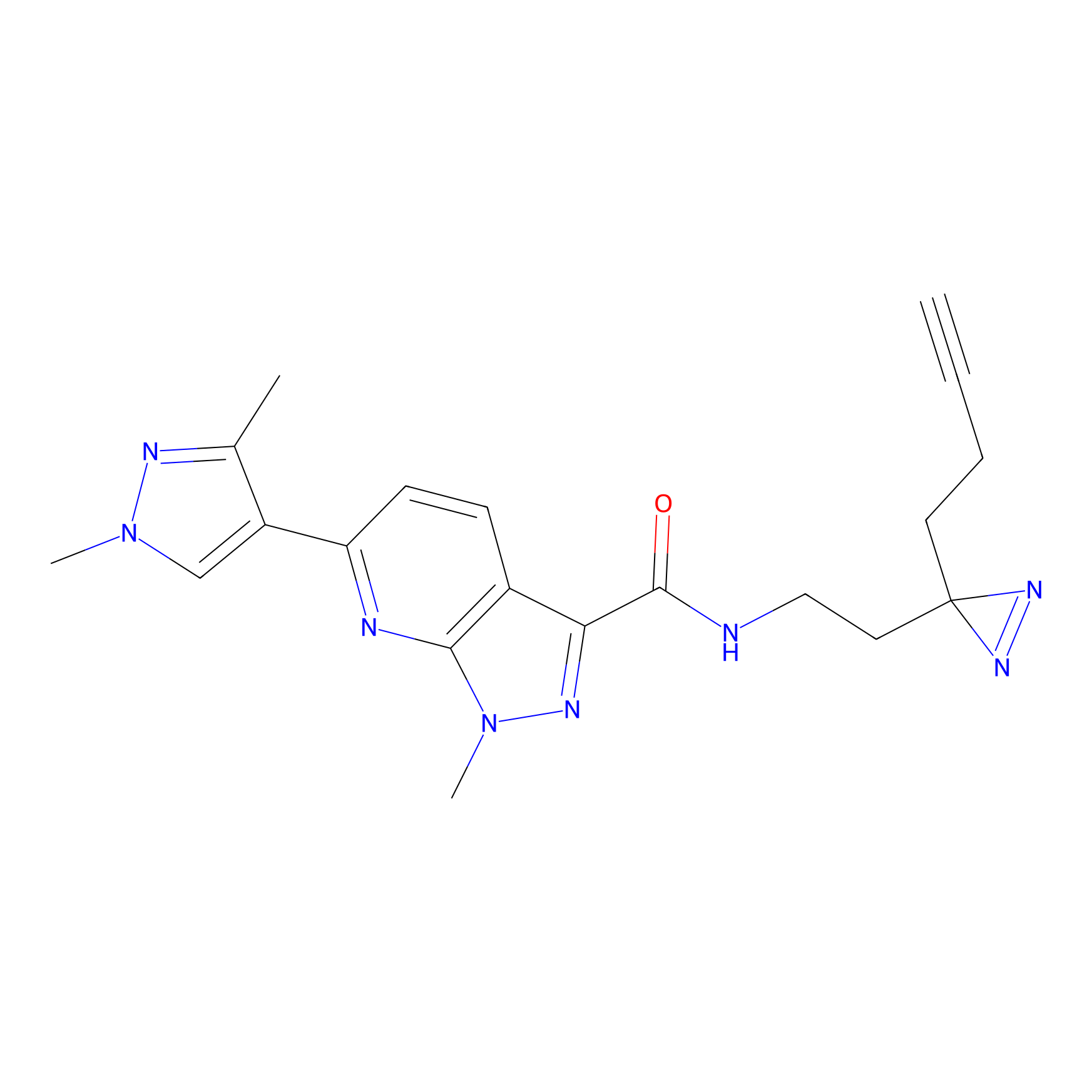
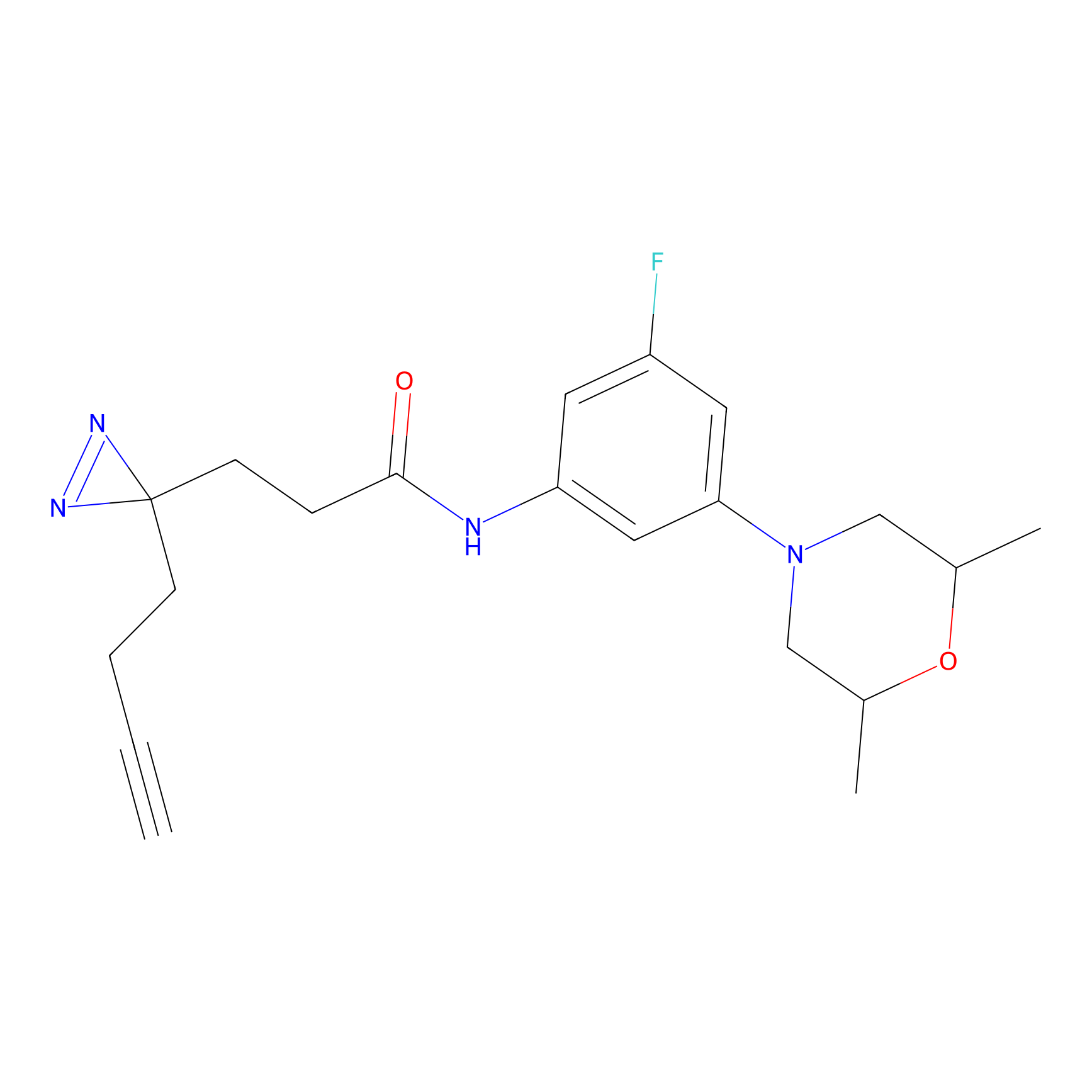
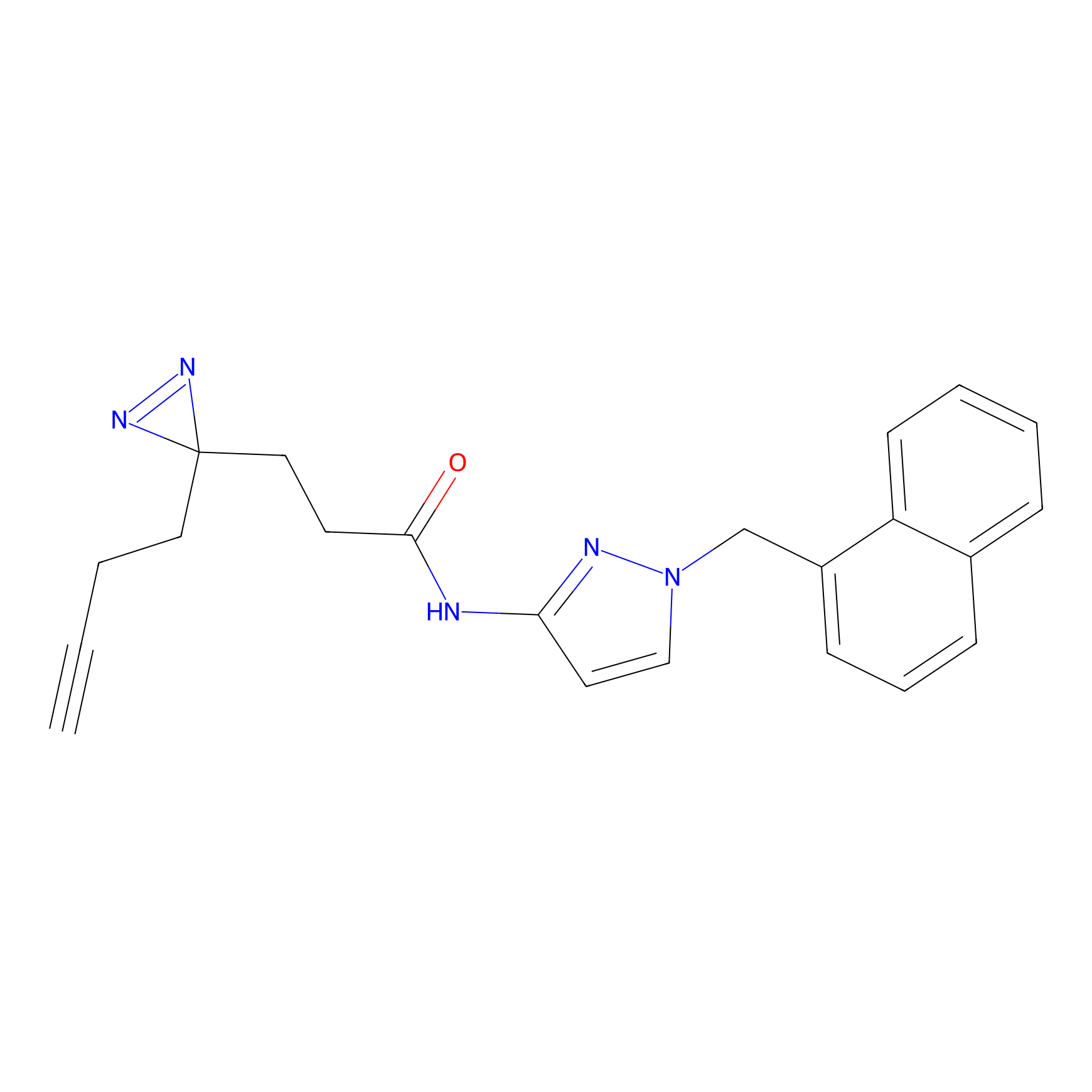
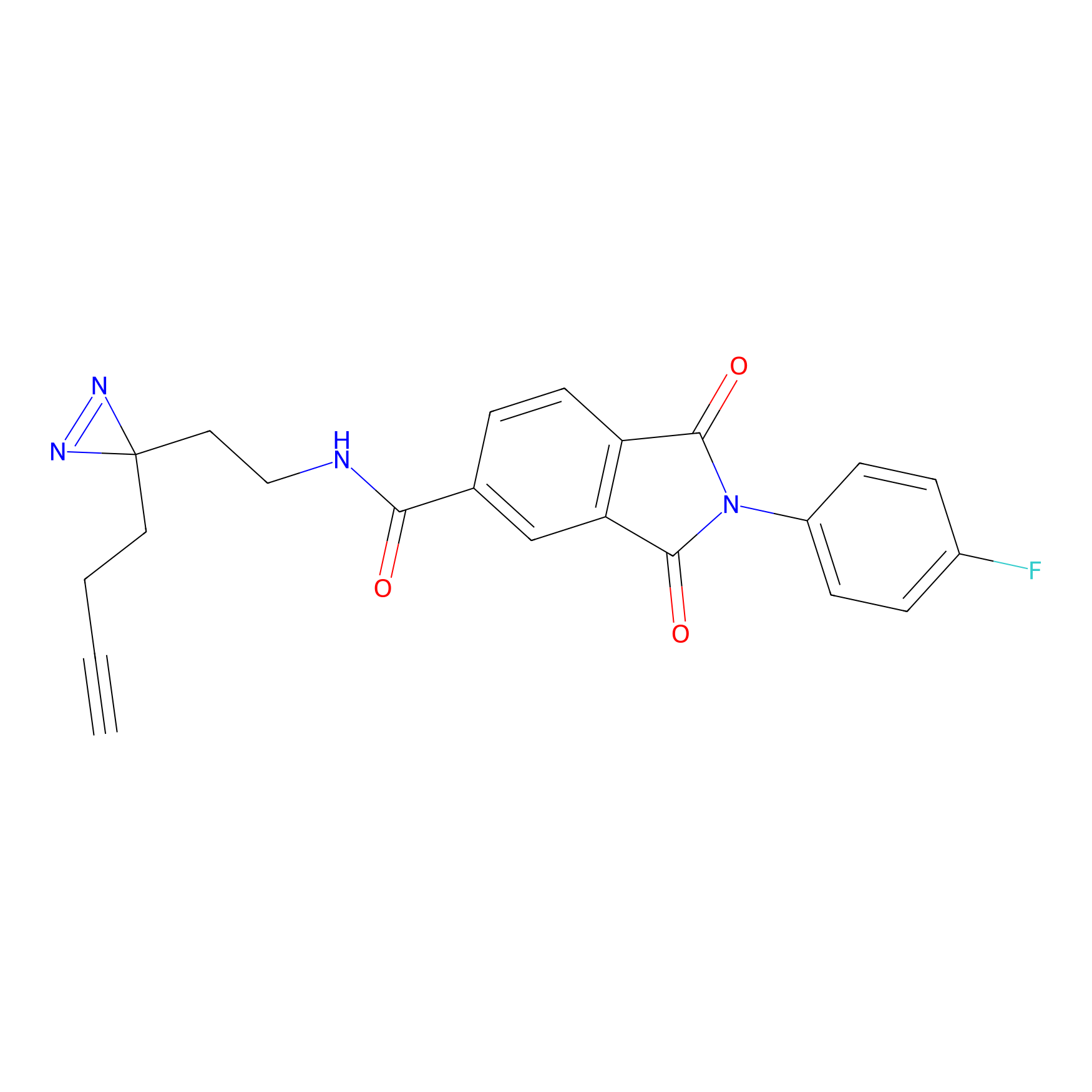
ABPP Probe
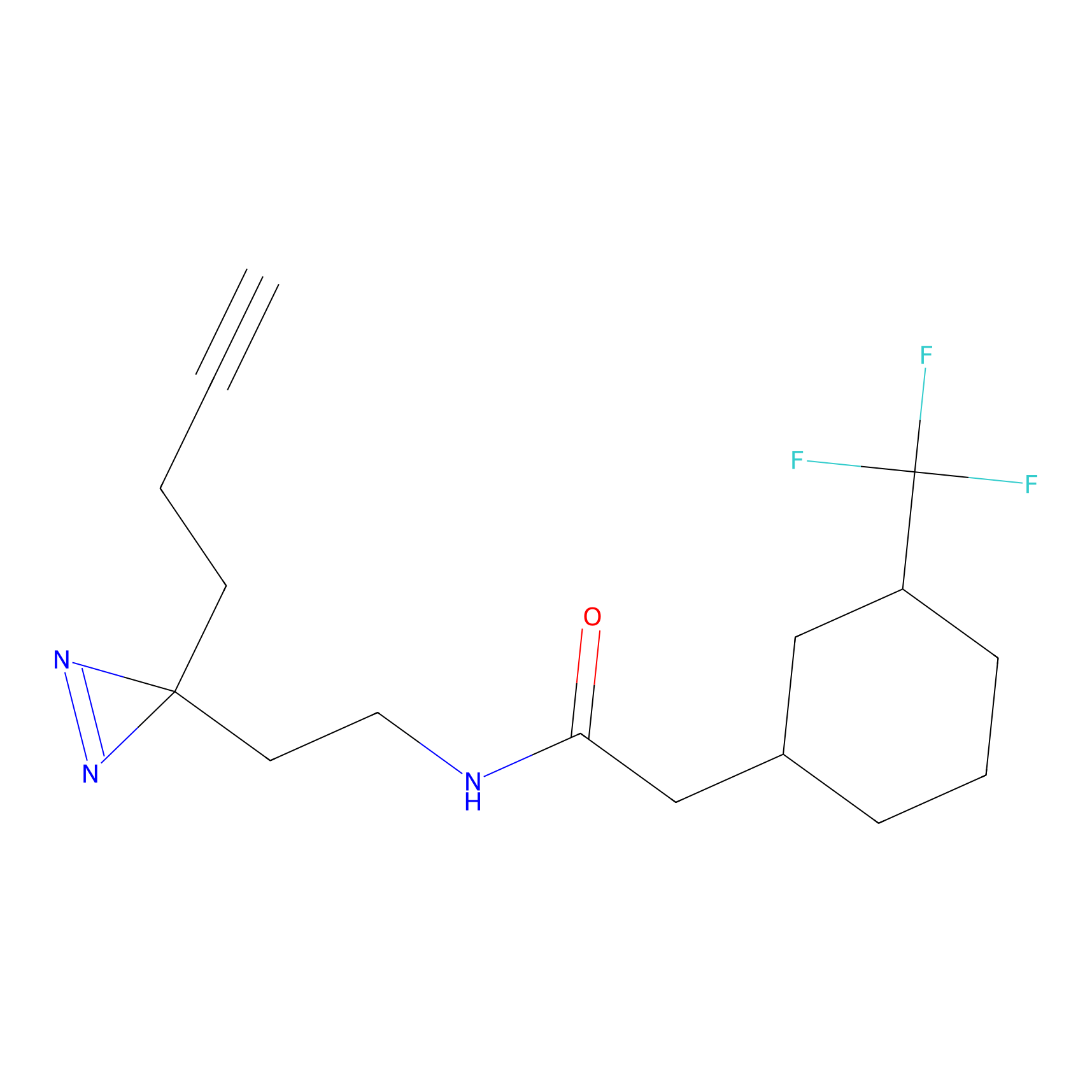
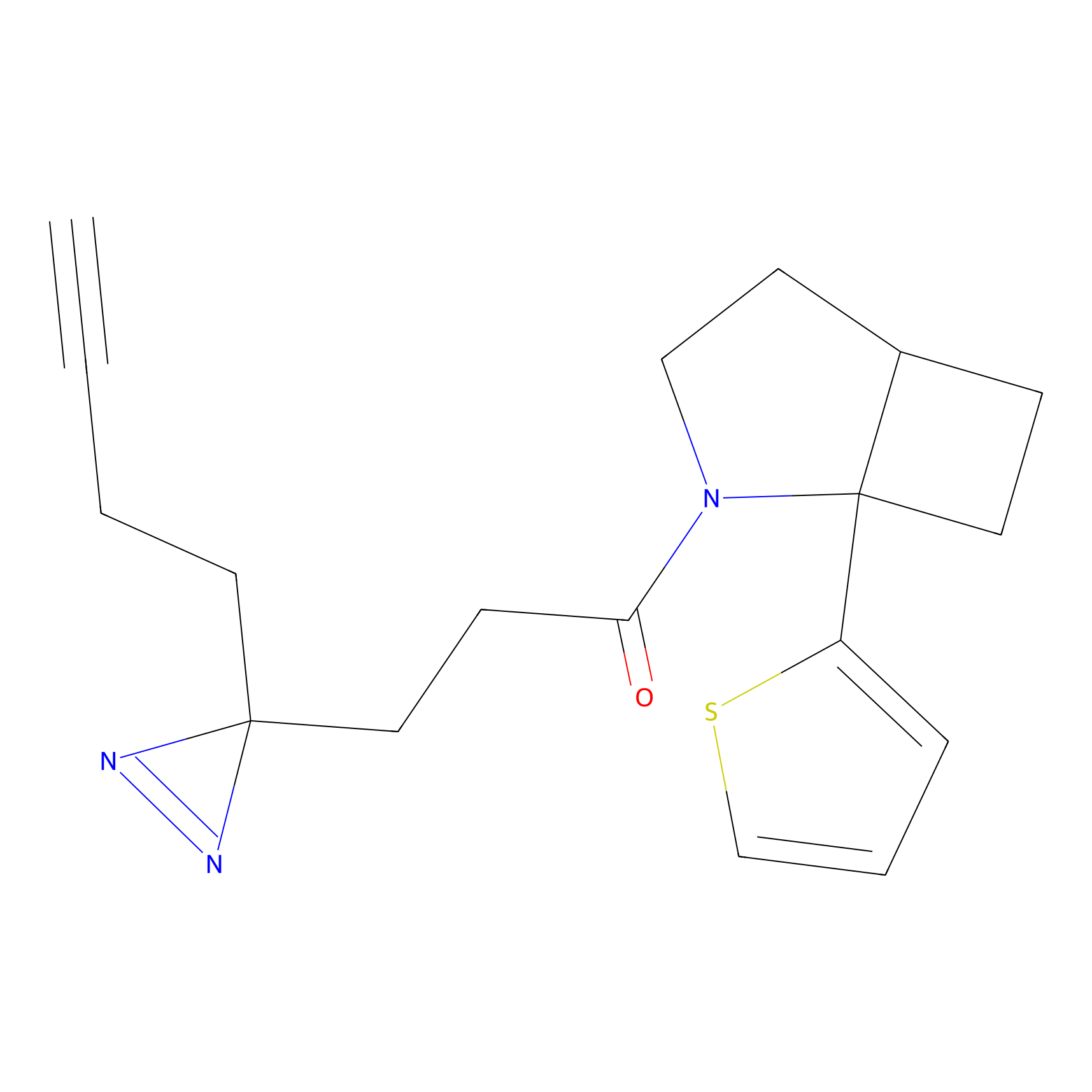
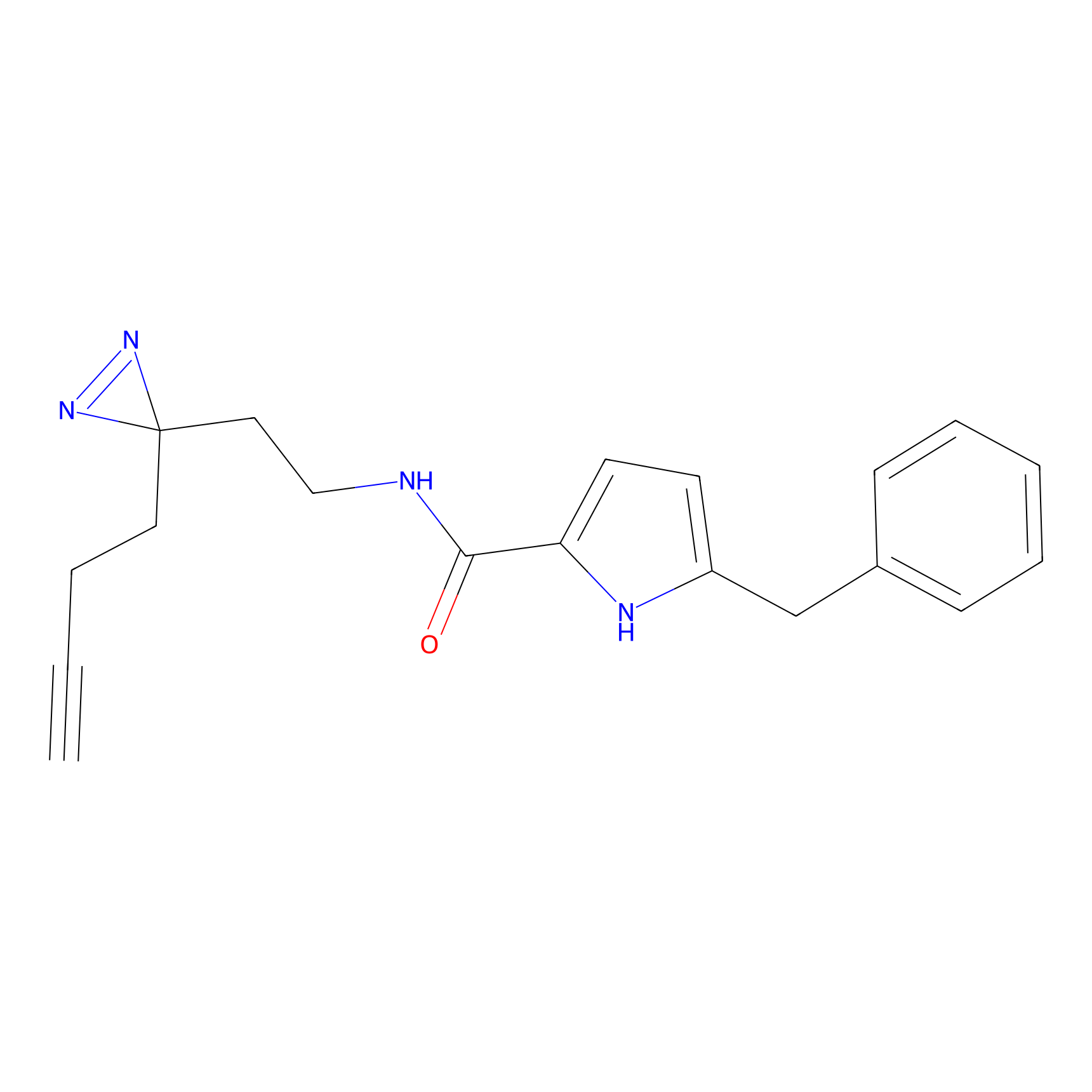
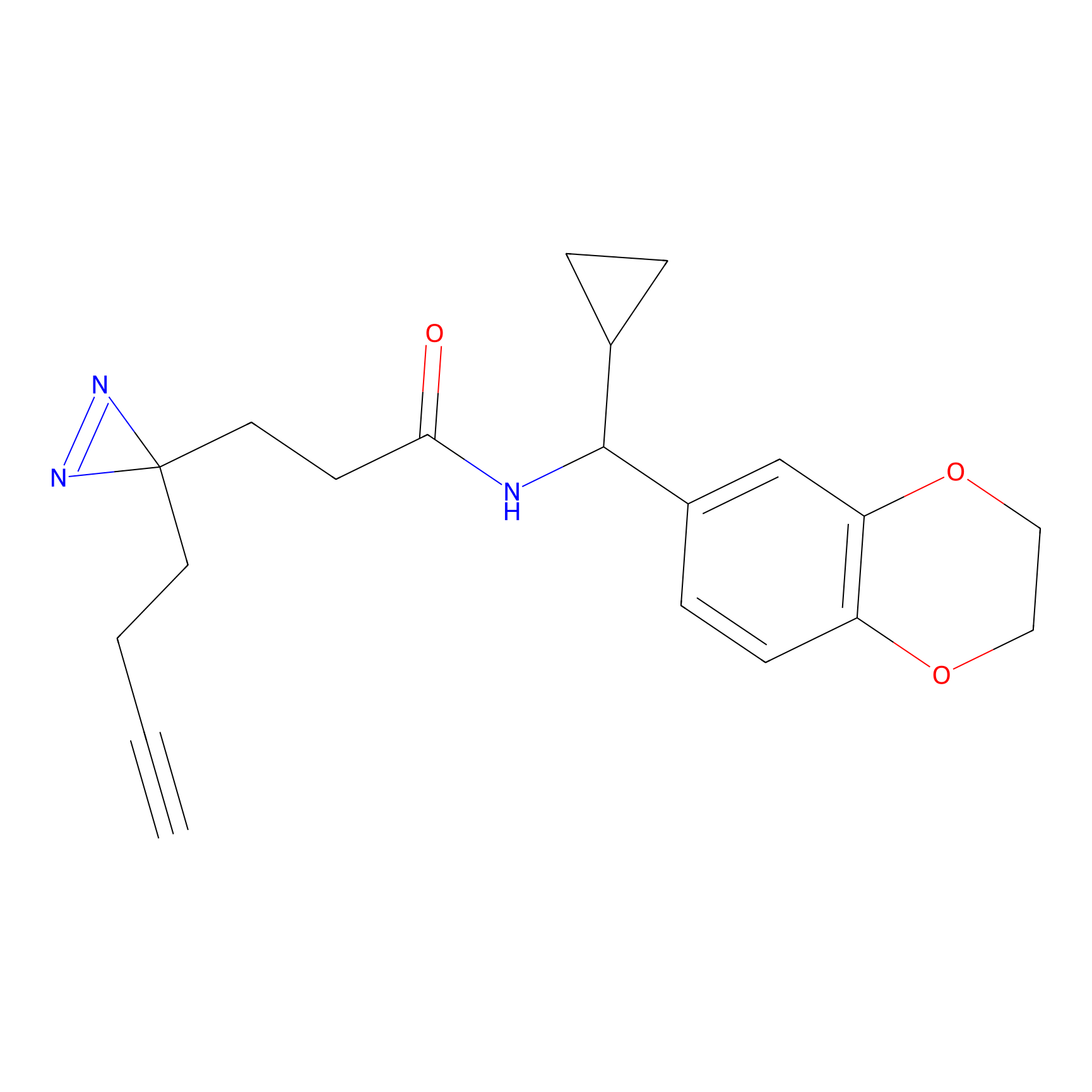
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
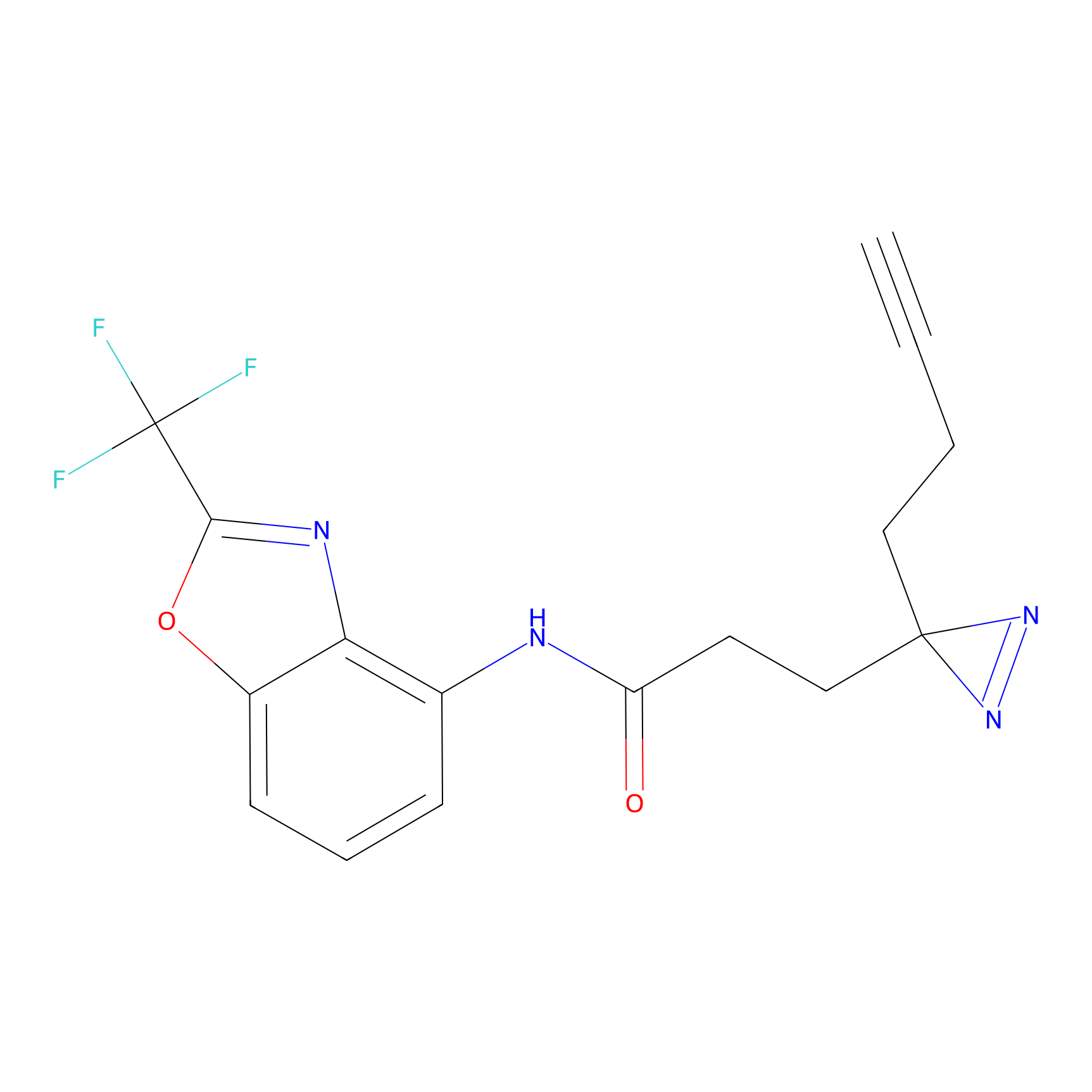
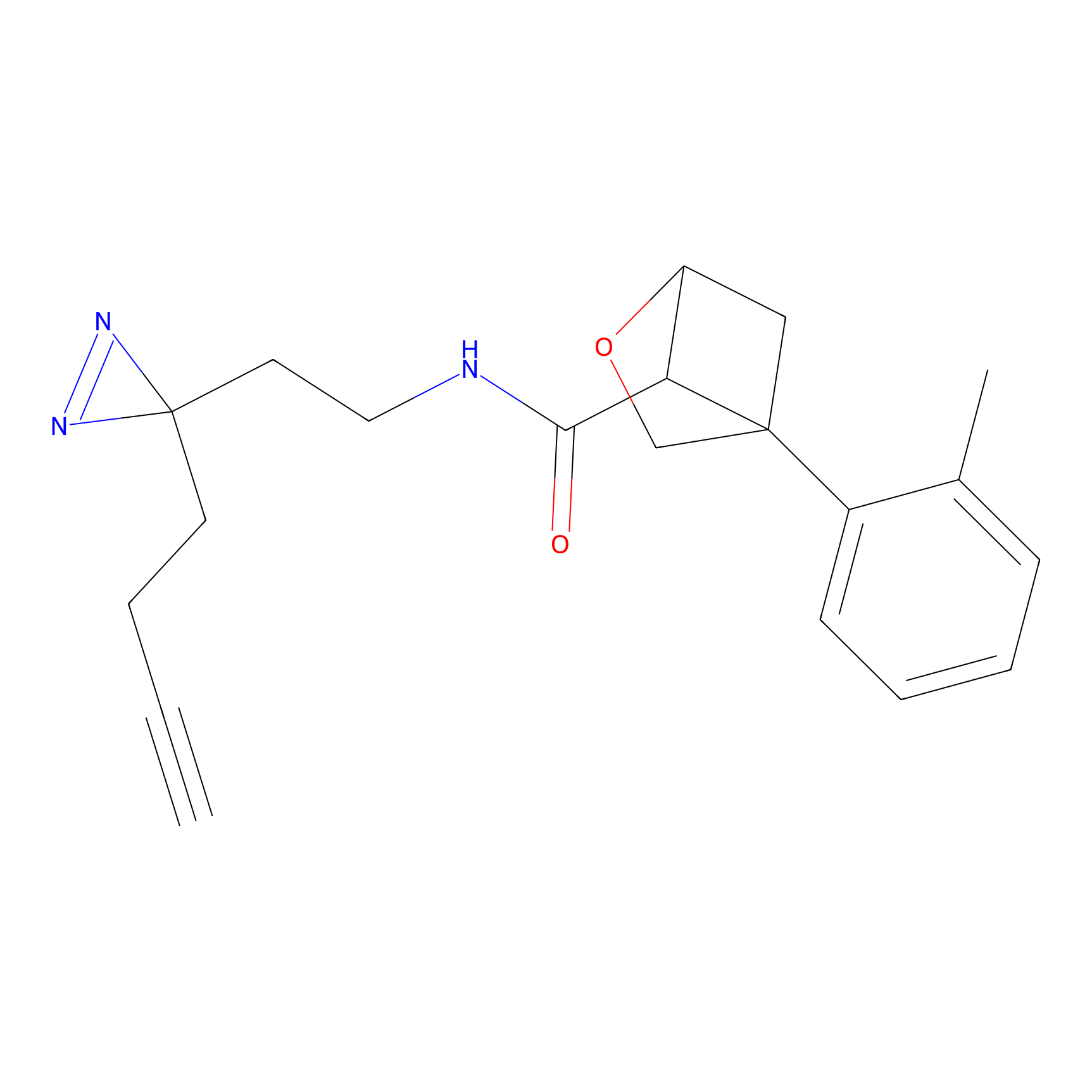
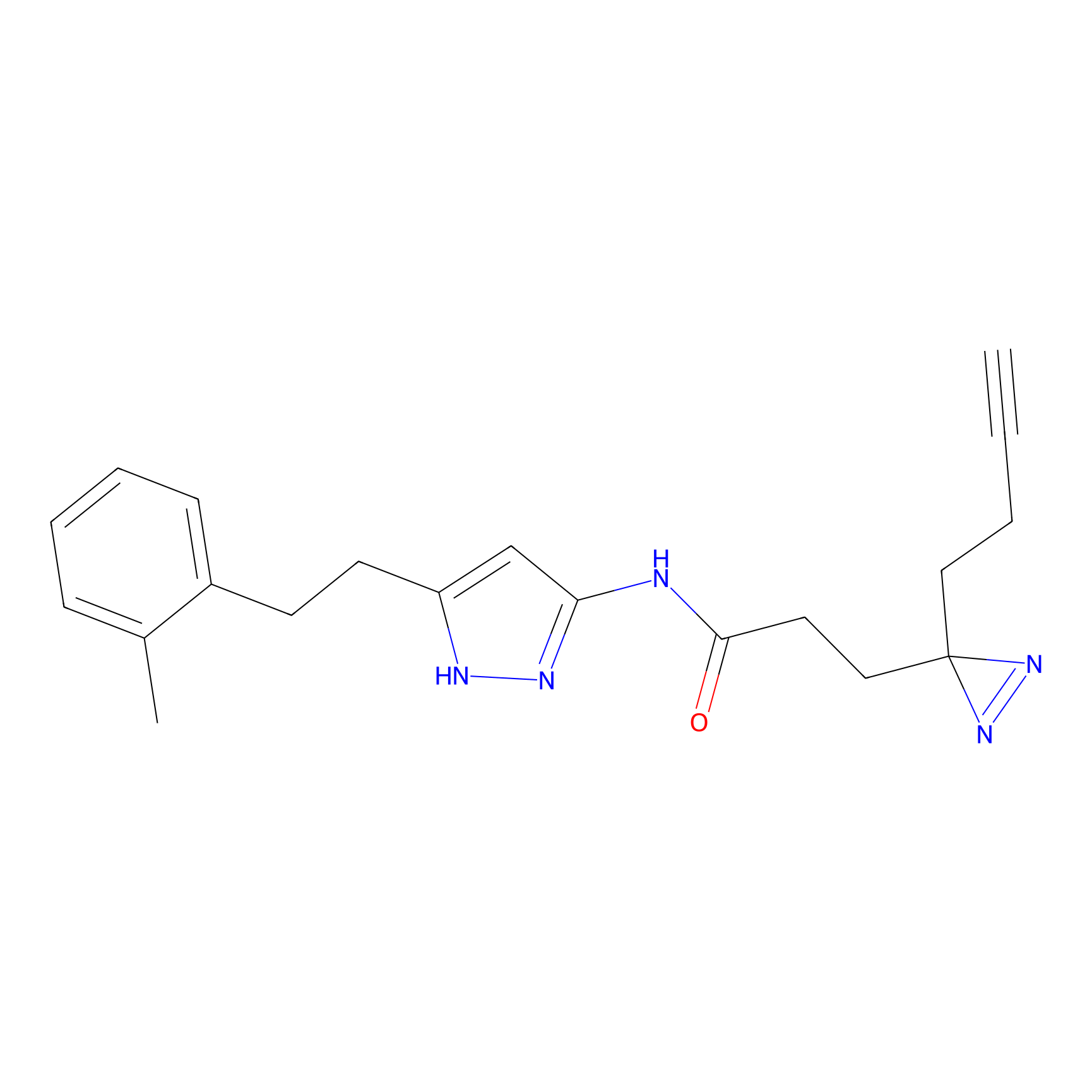
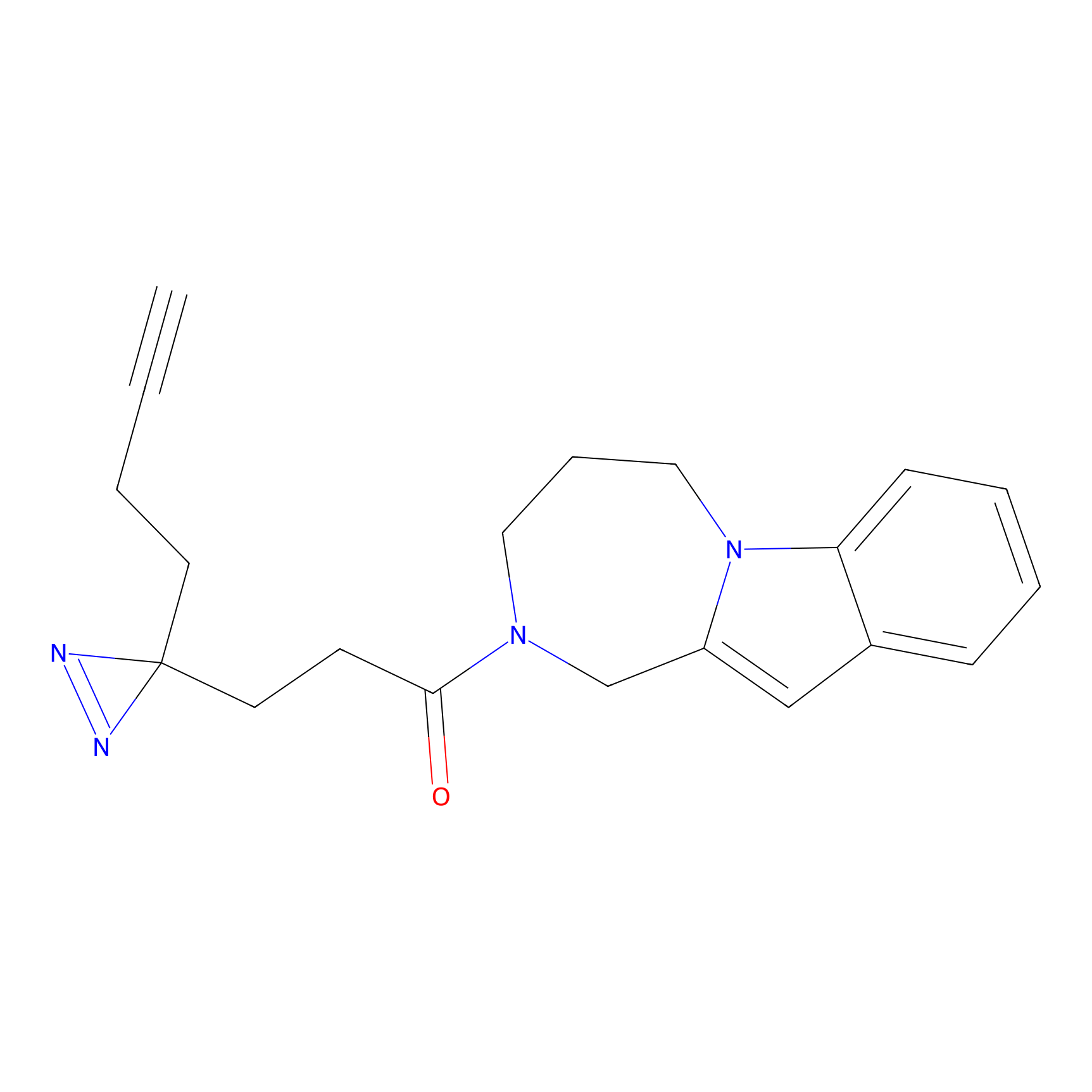
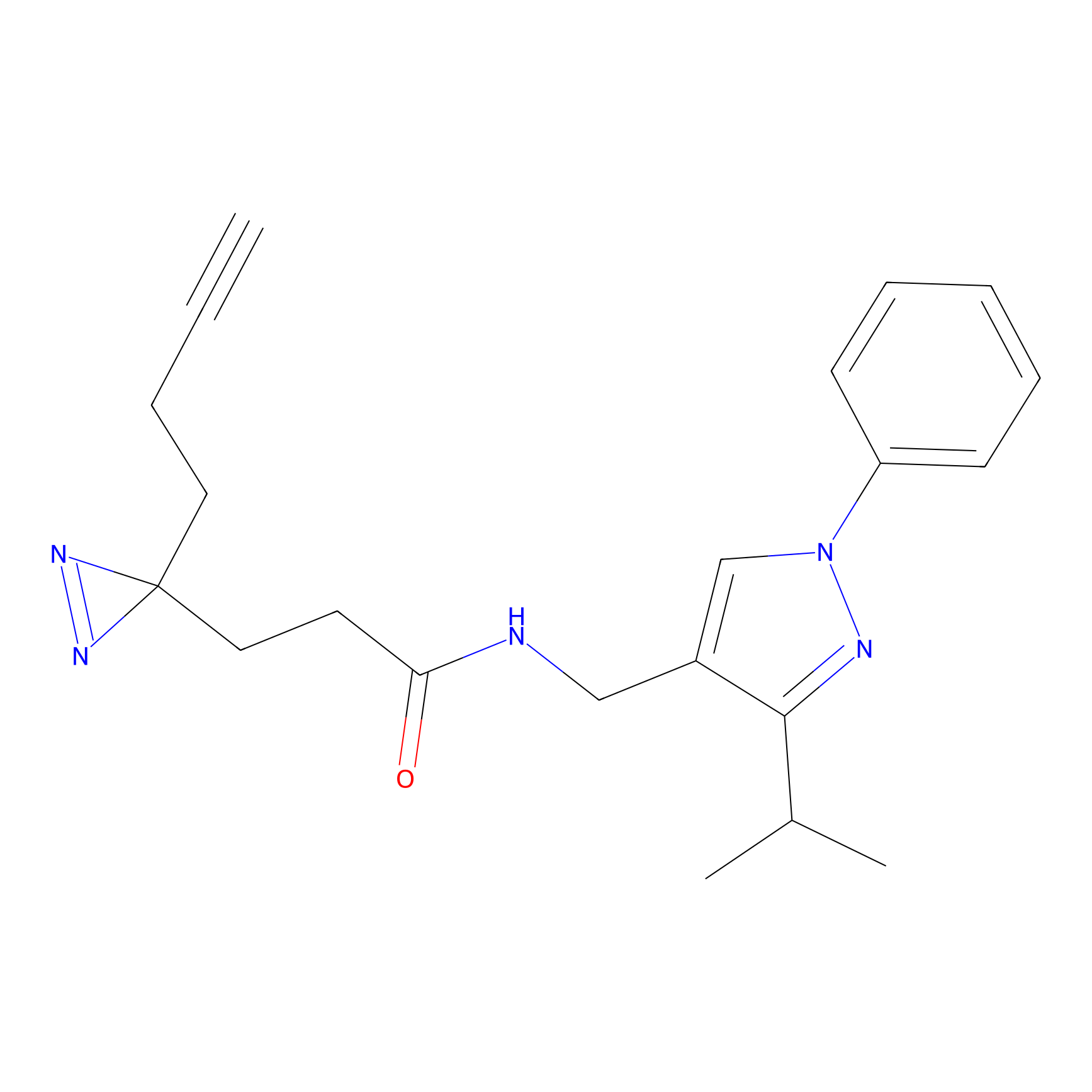
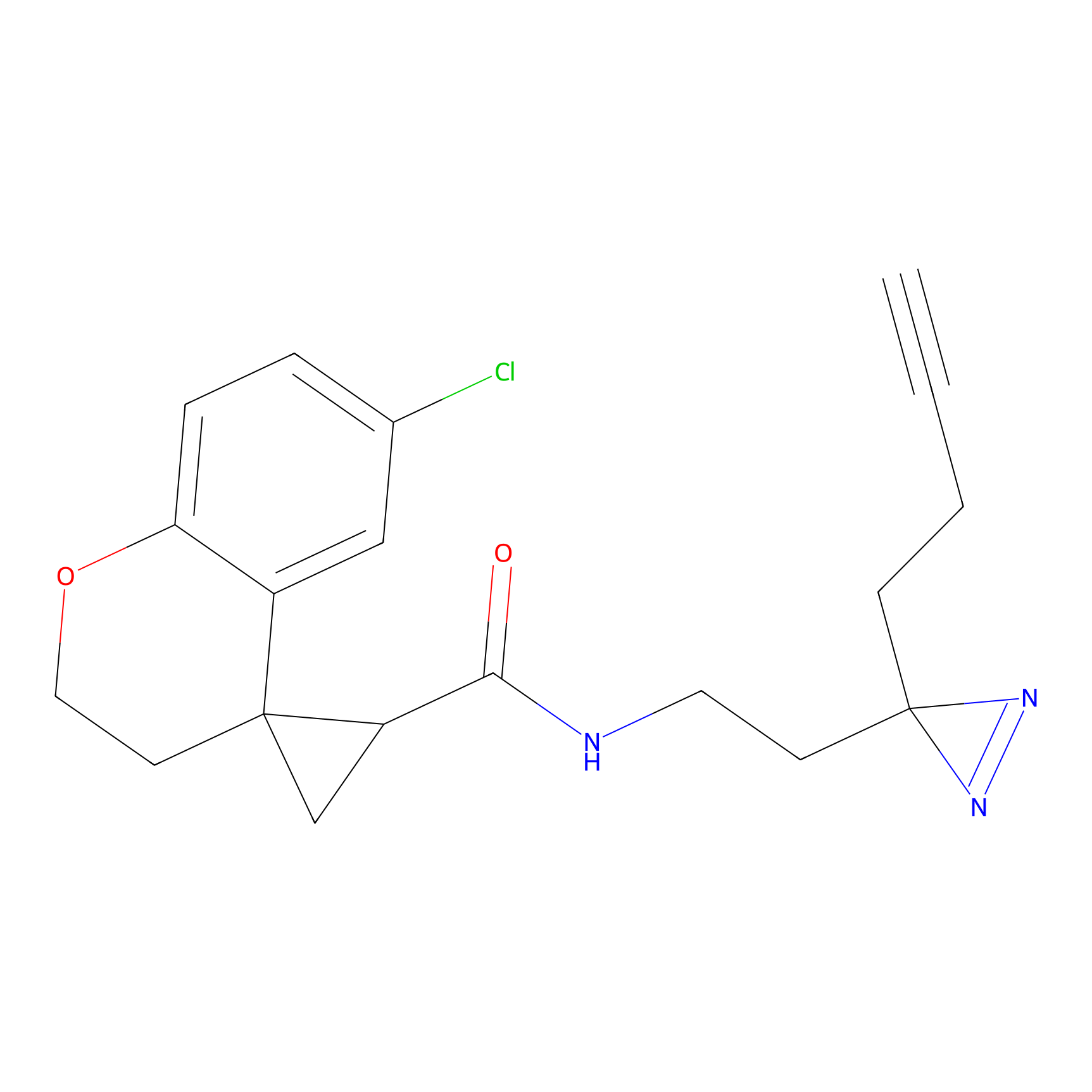
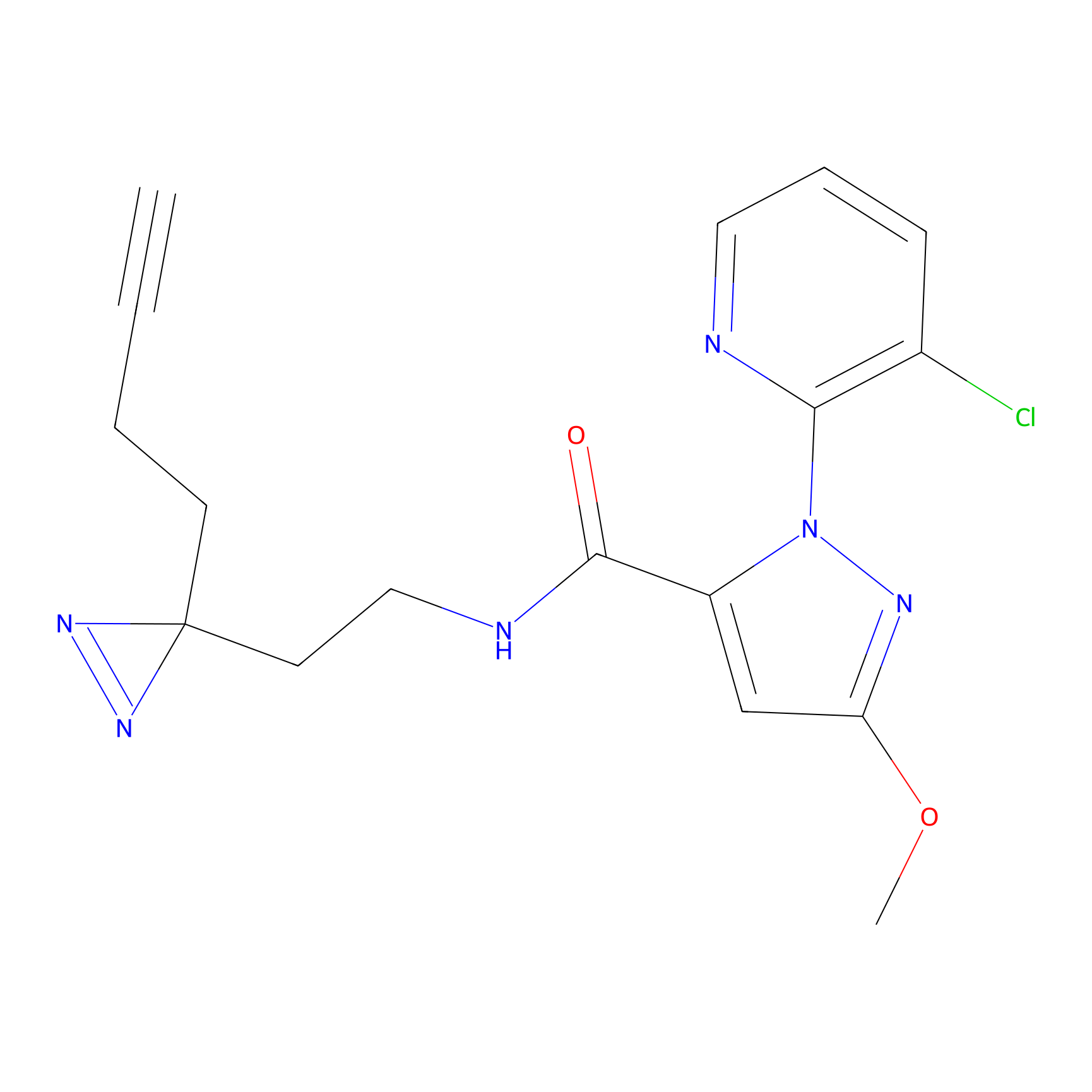
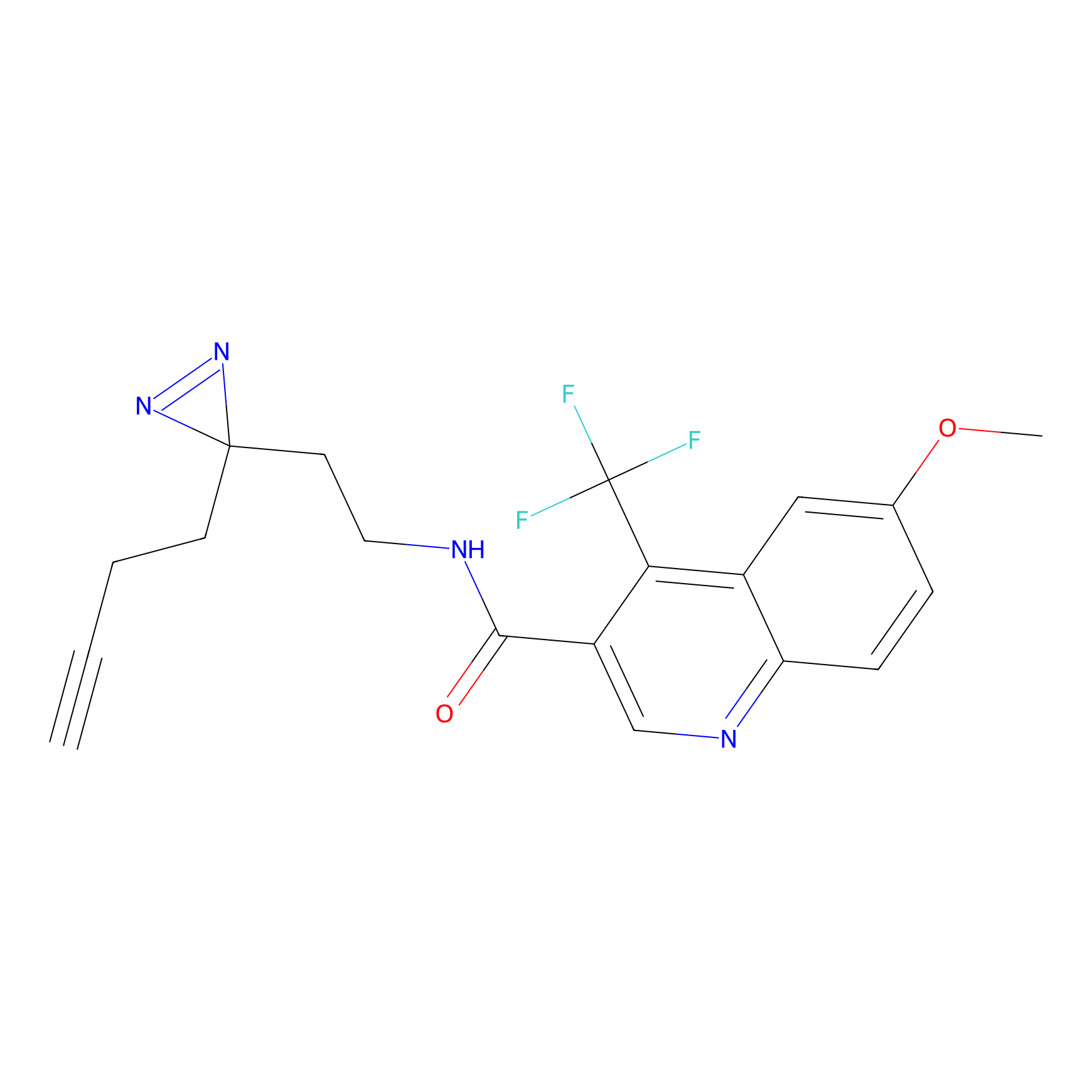
|
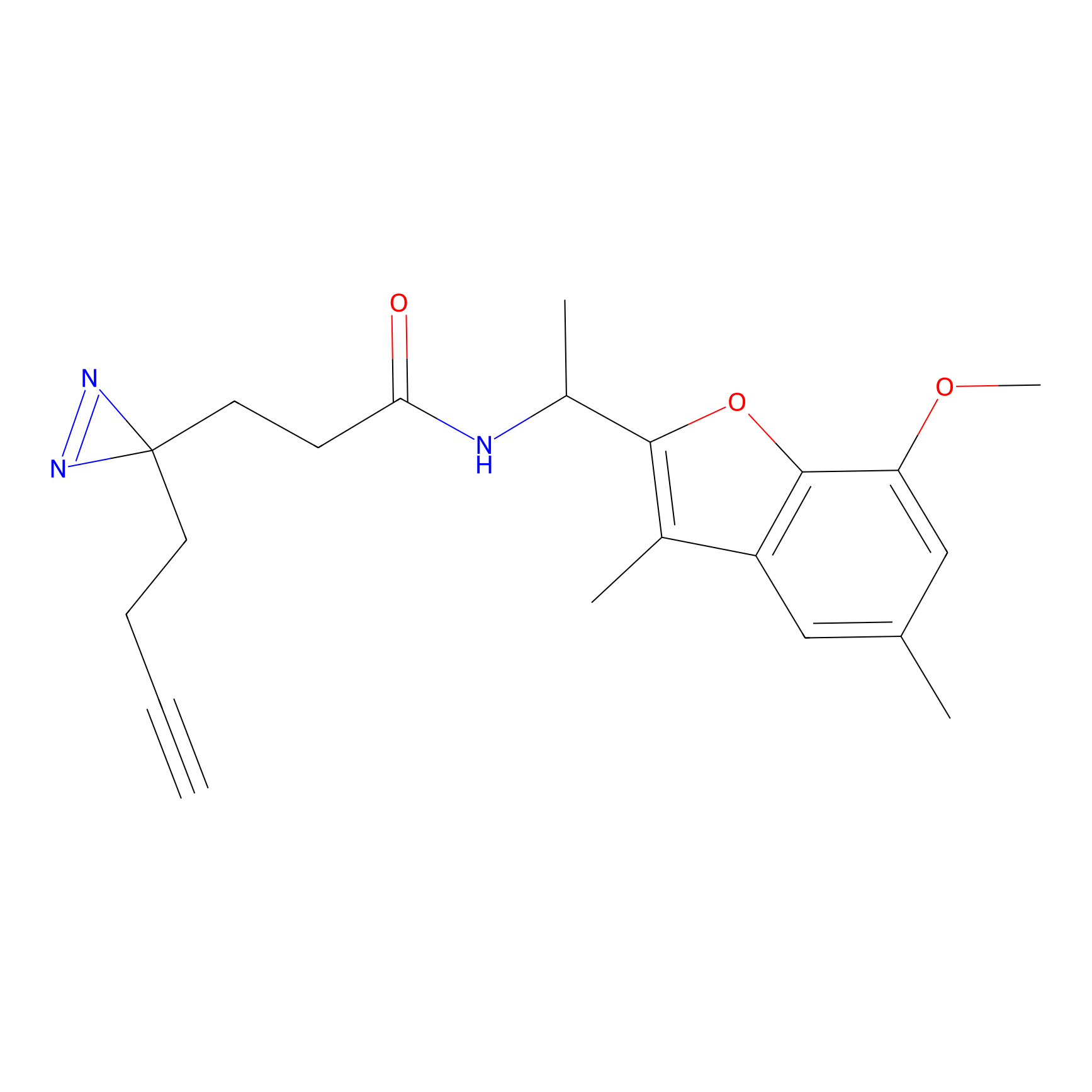
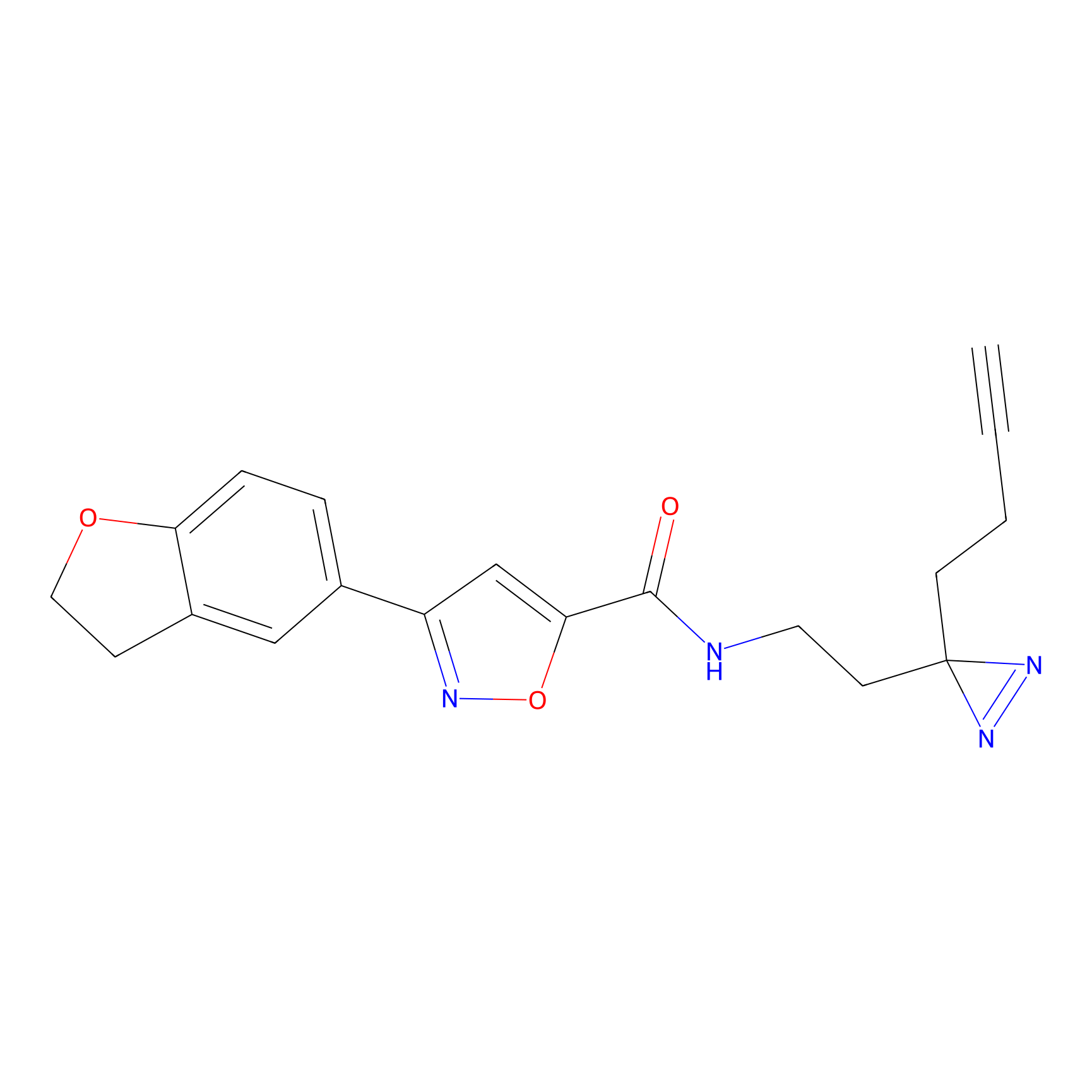
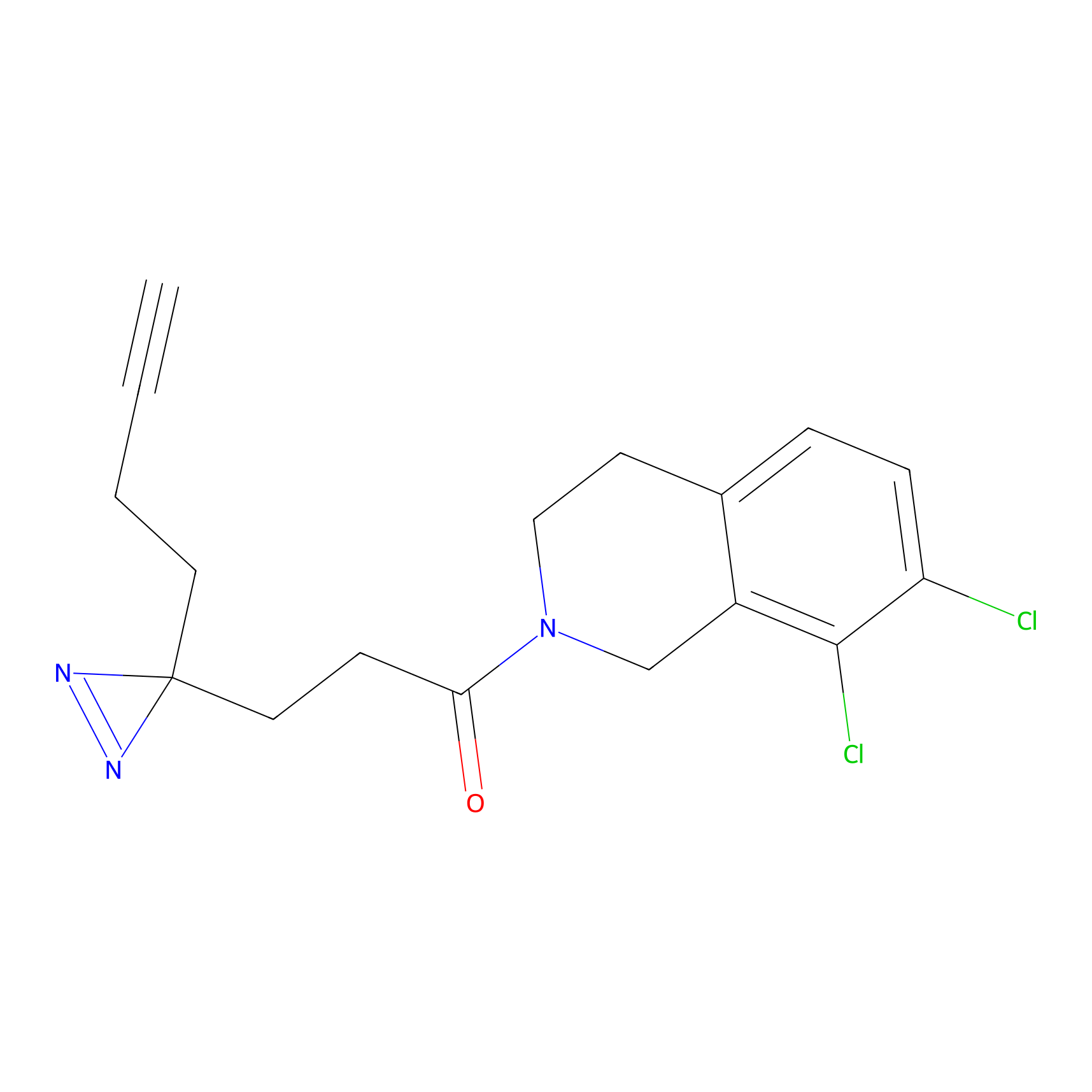
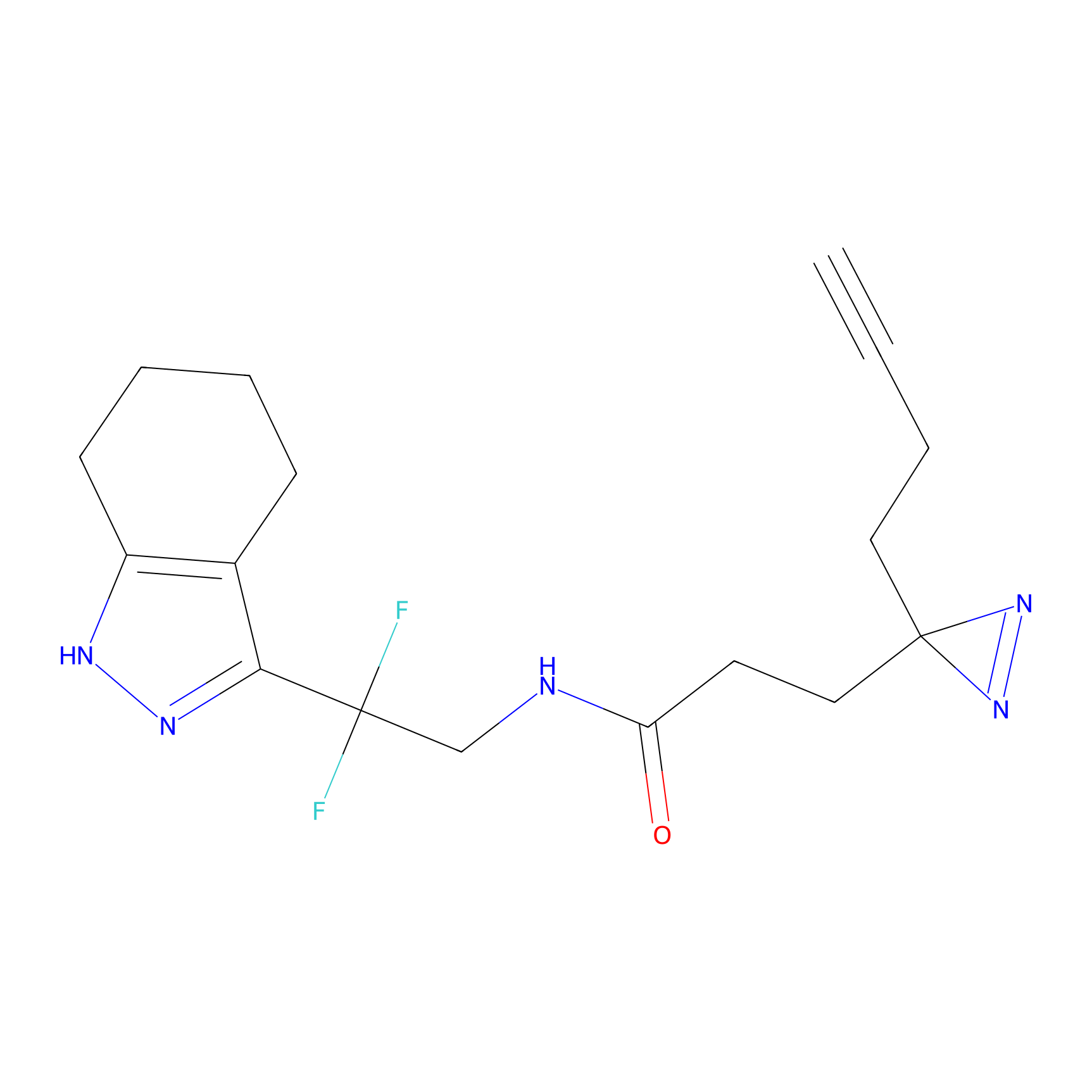
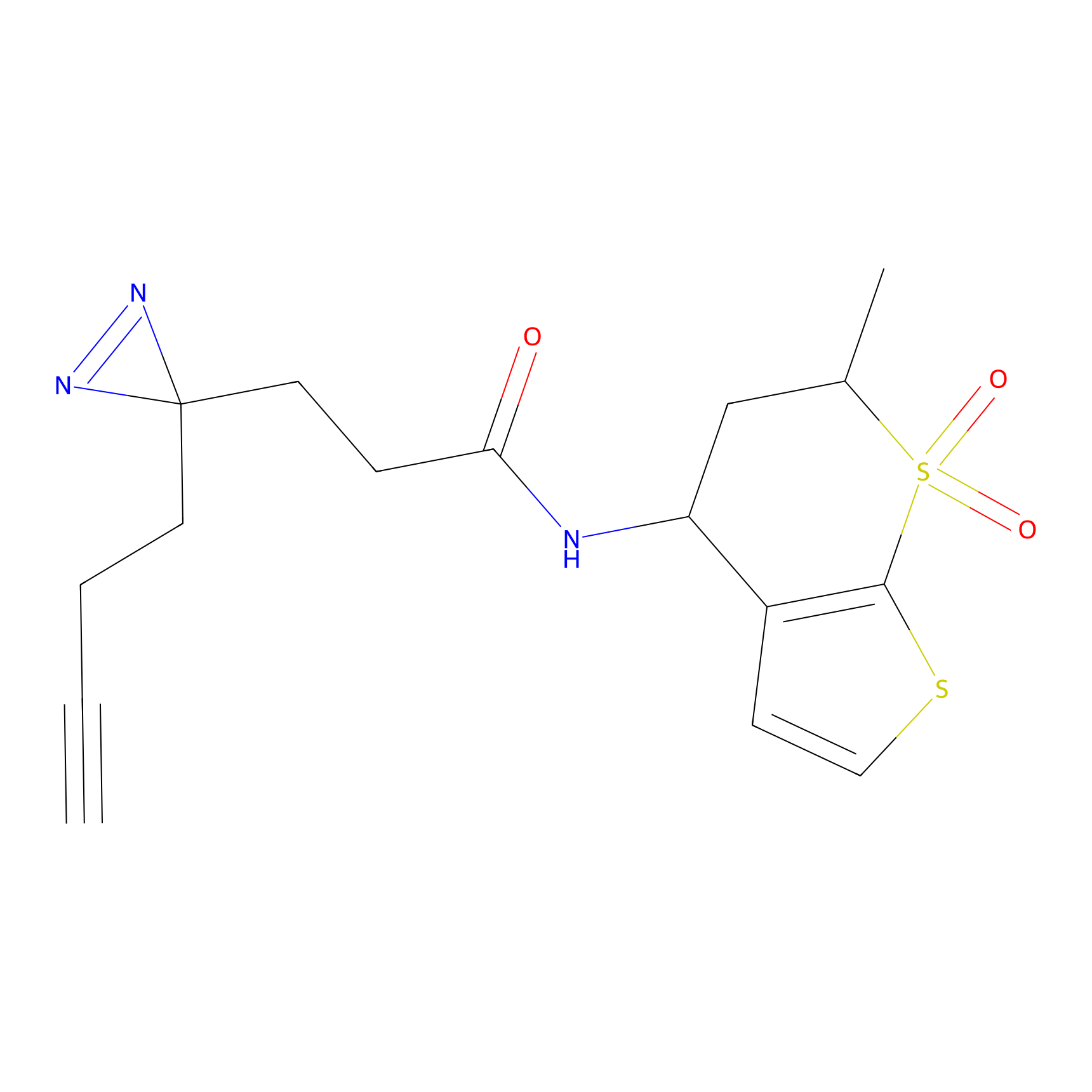
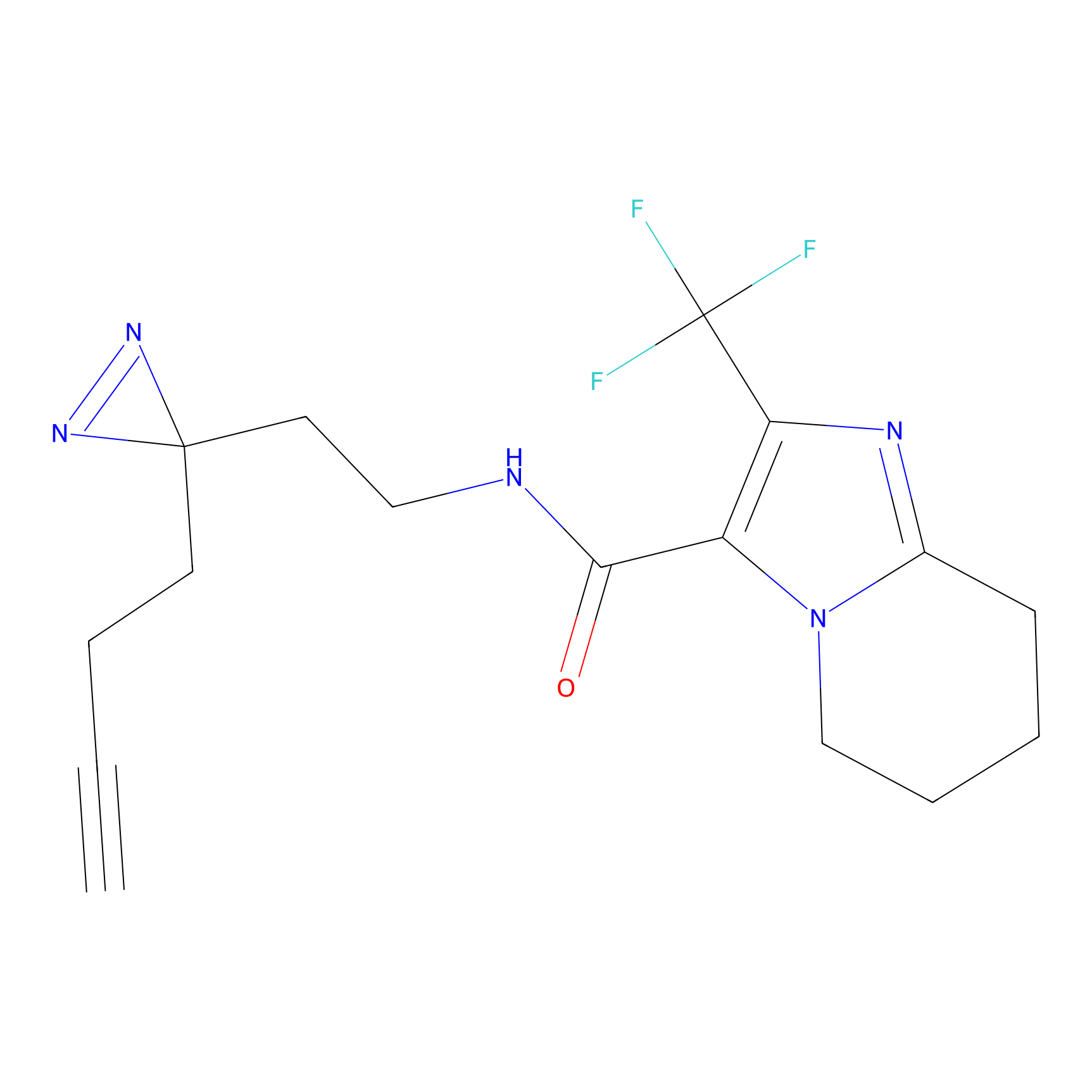
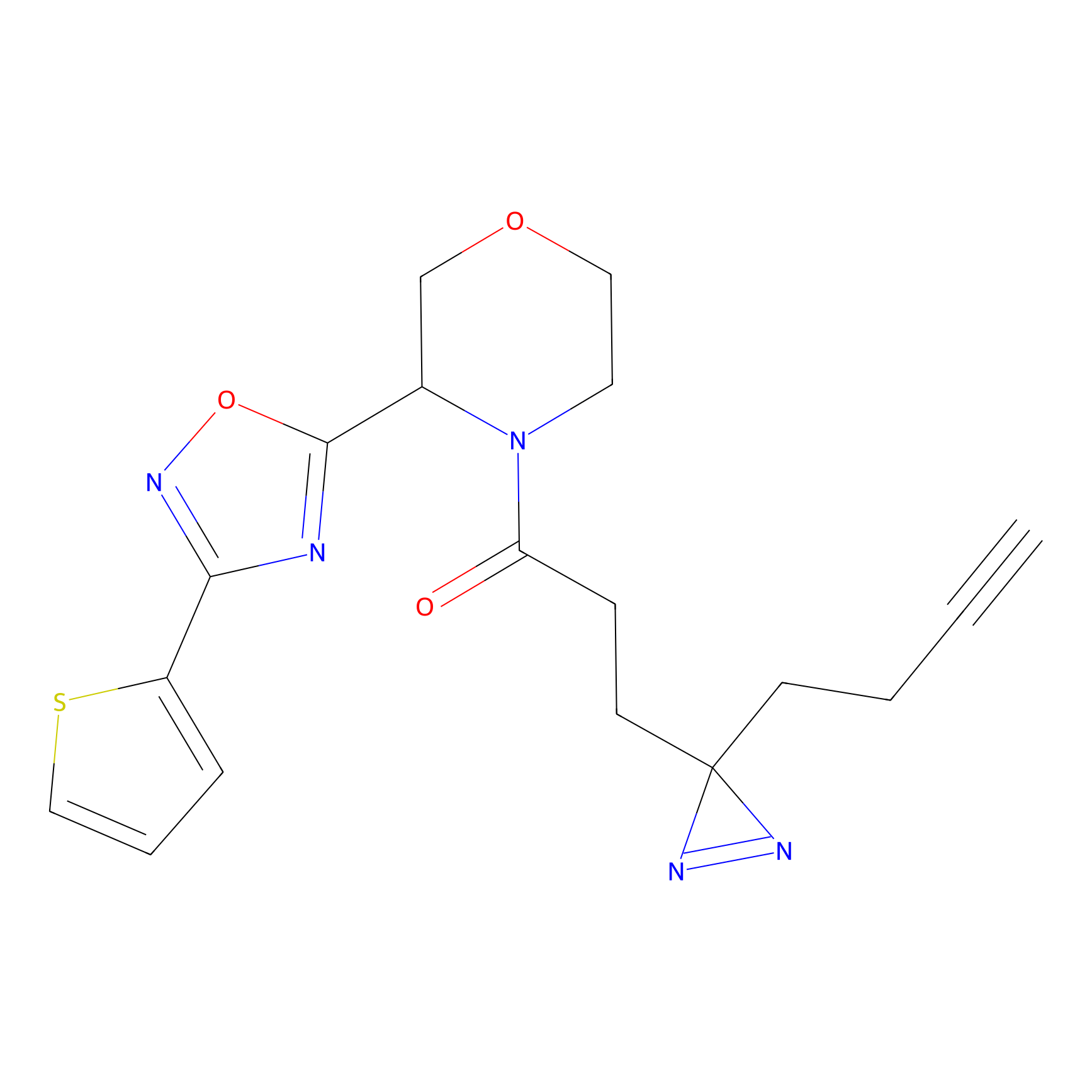
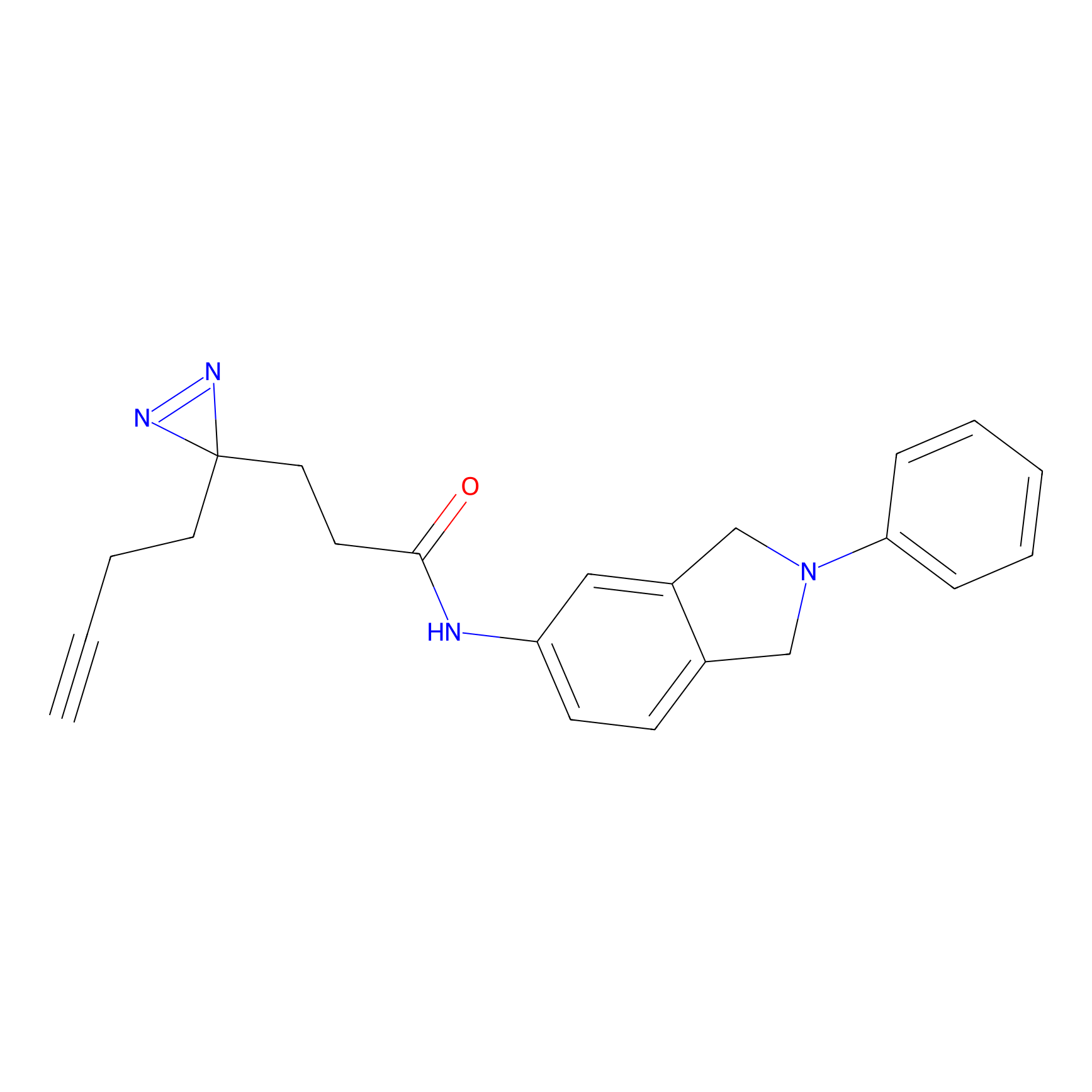
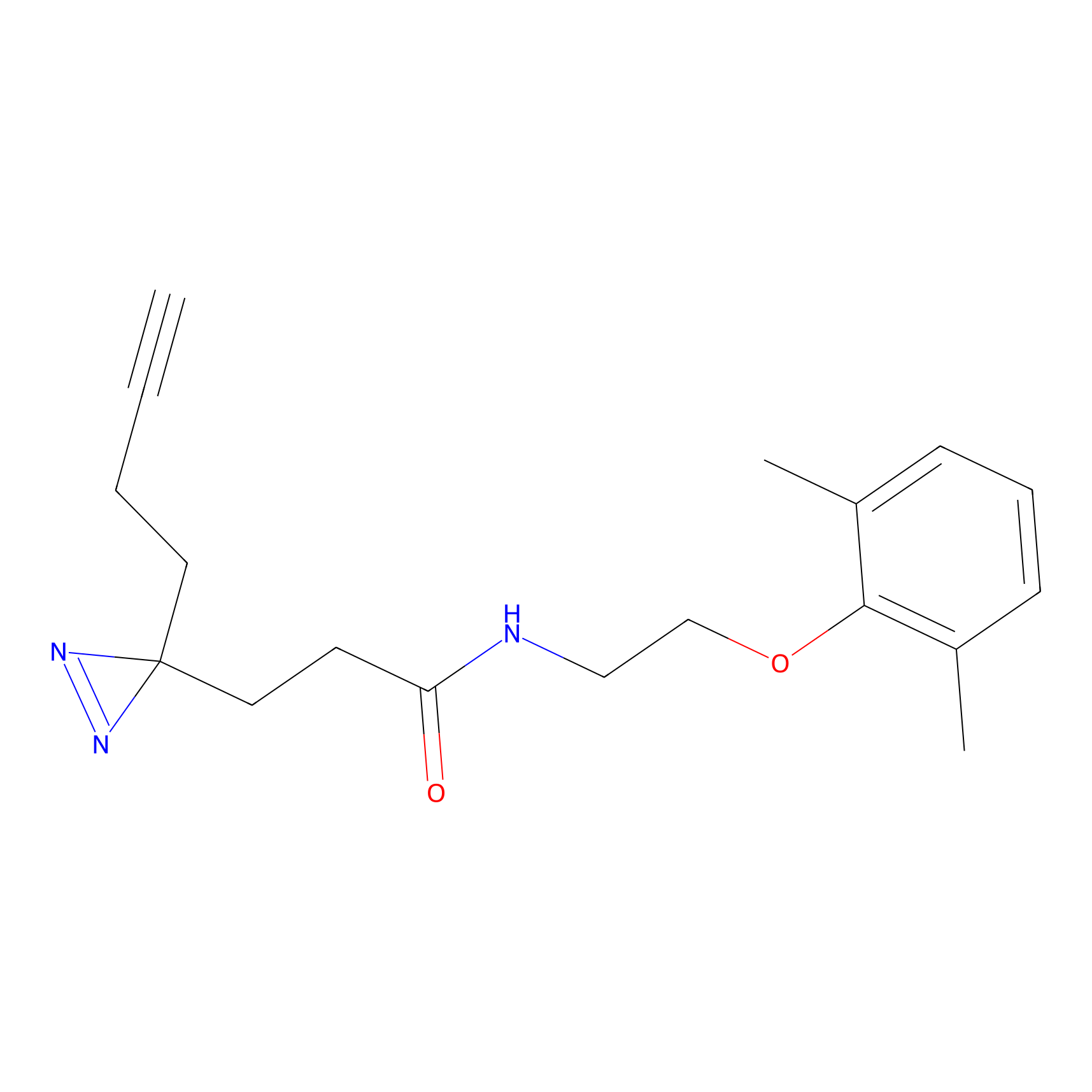
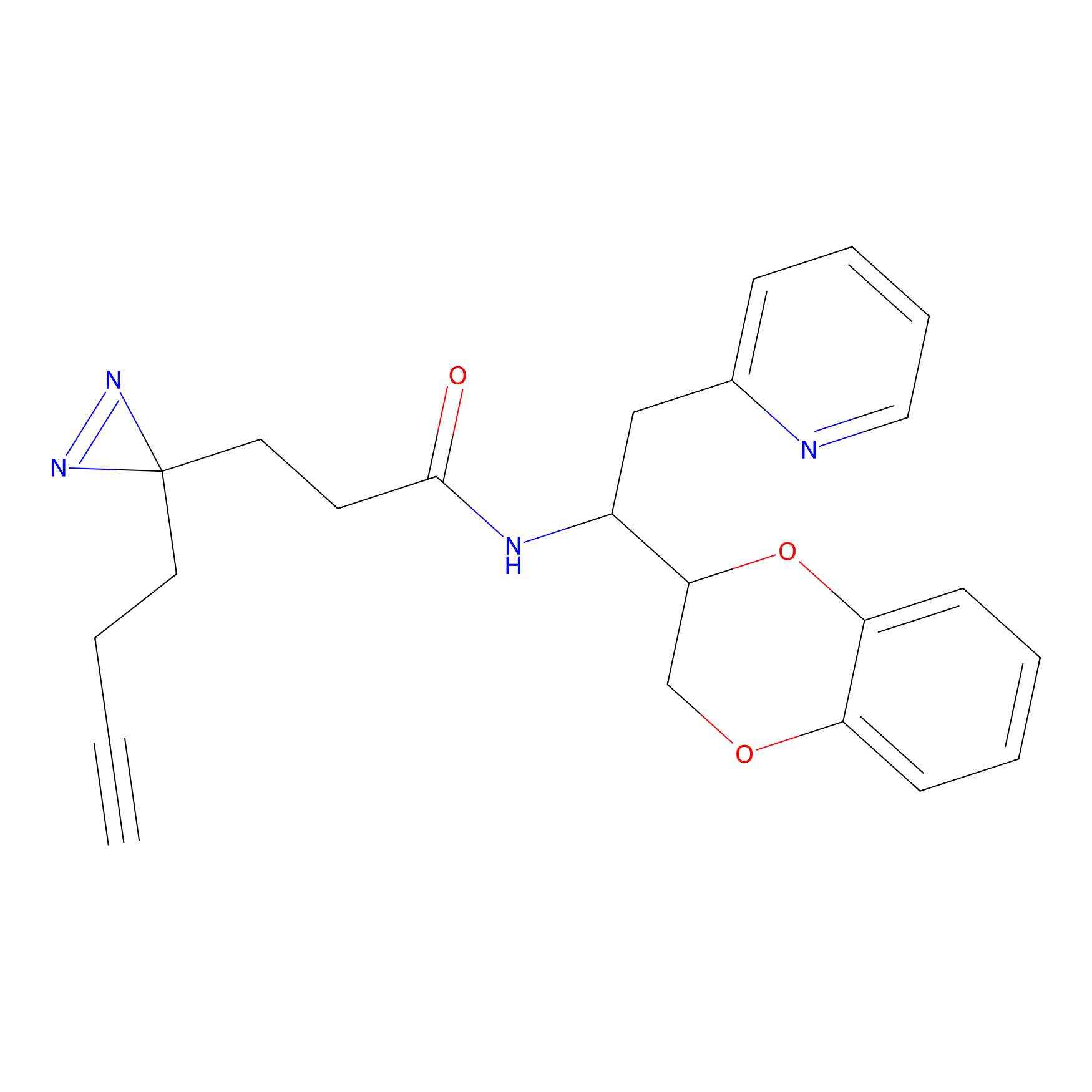
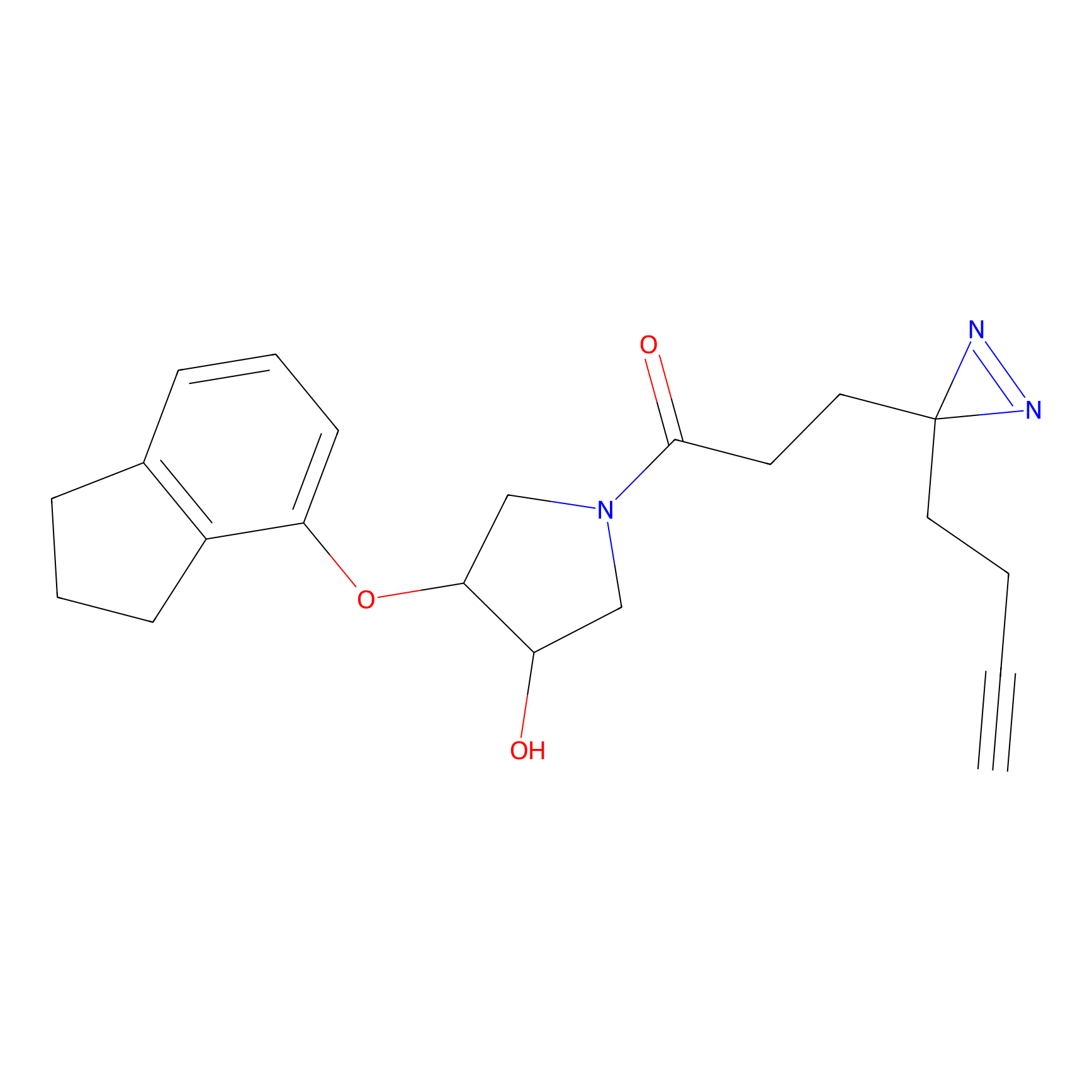
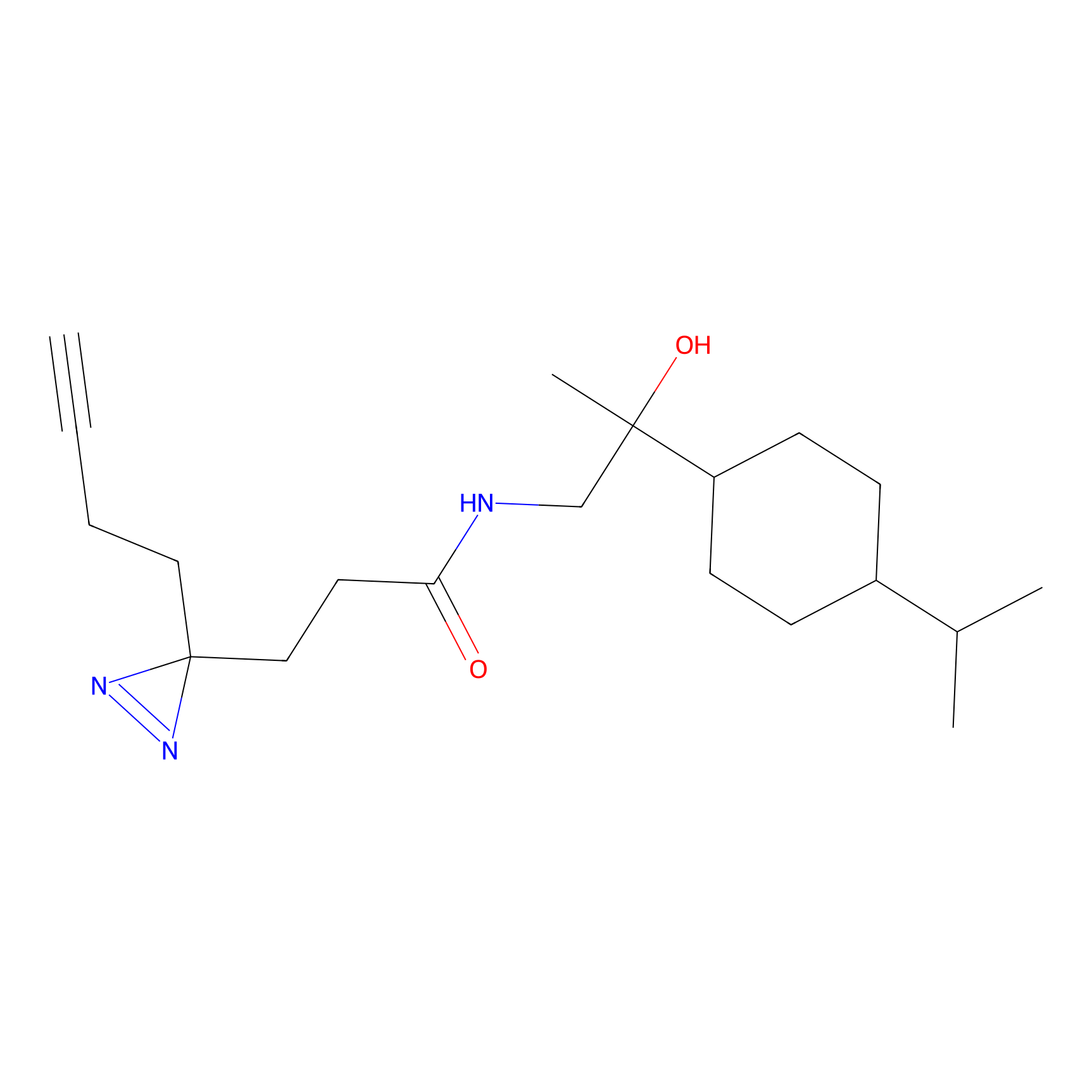
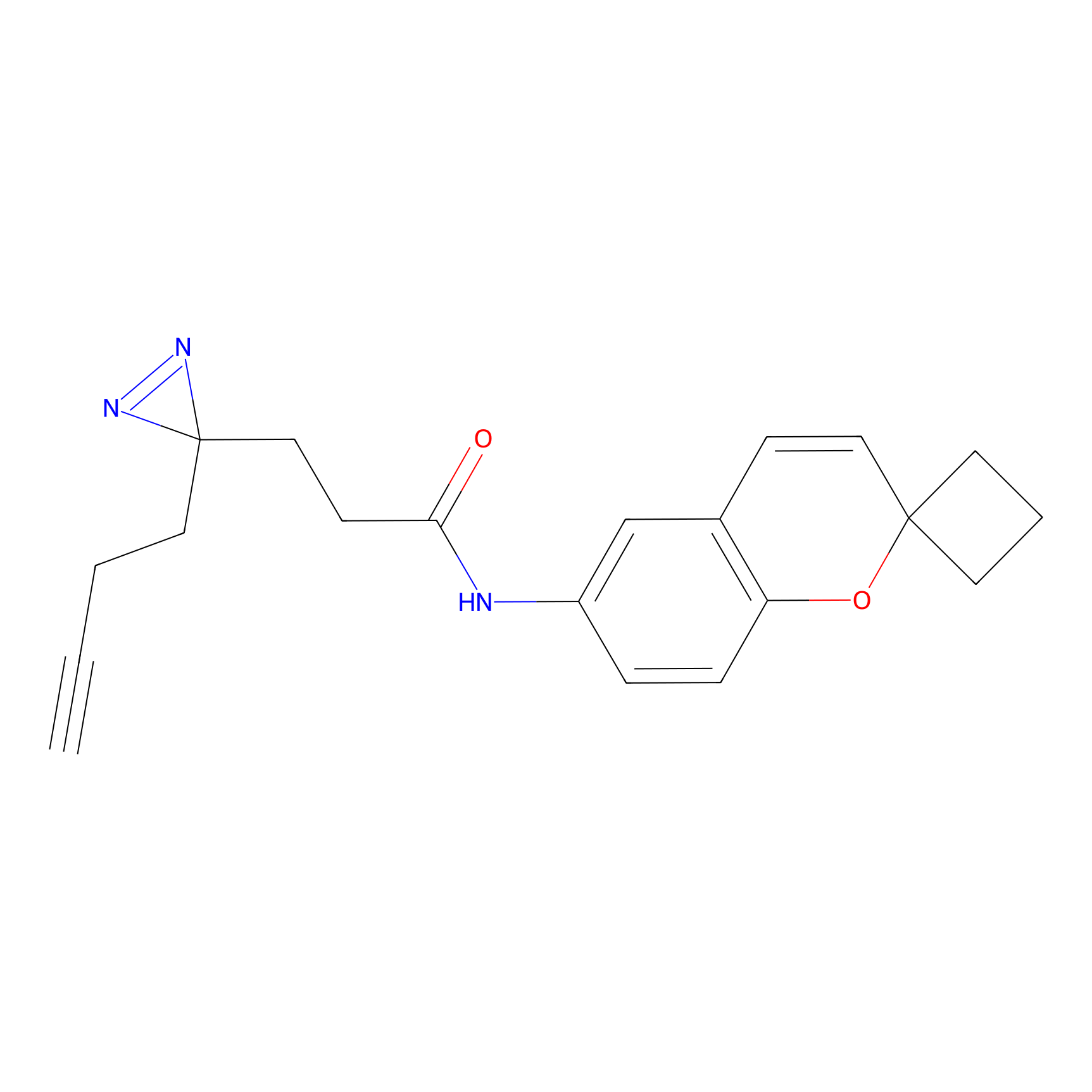
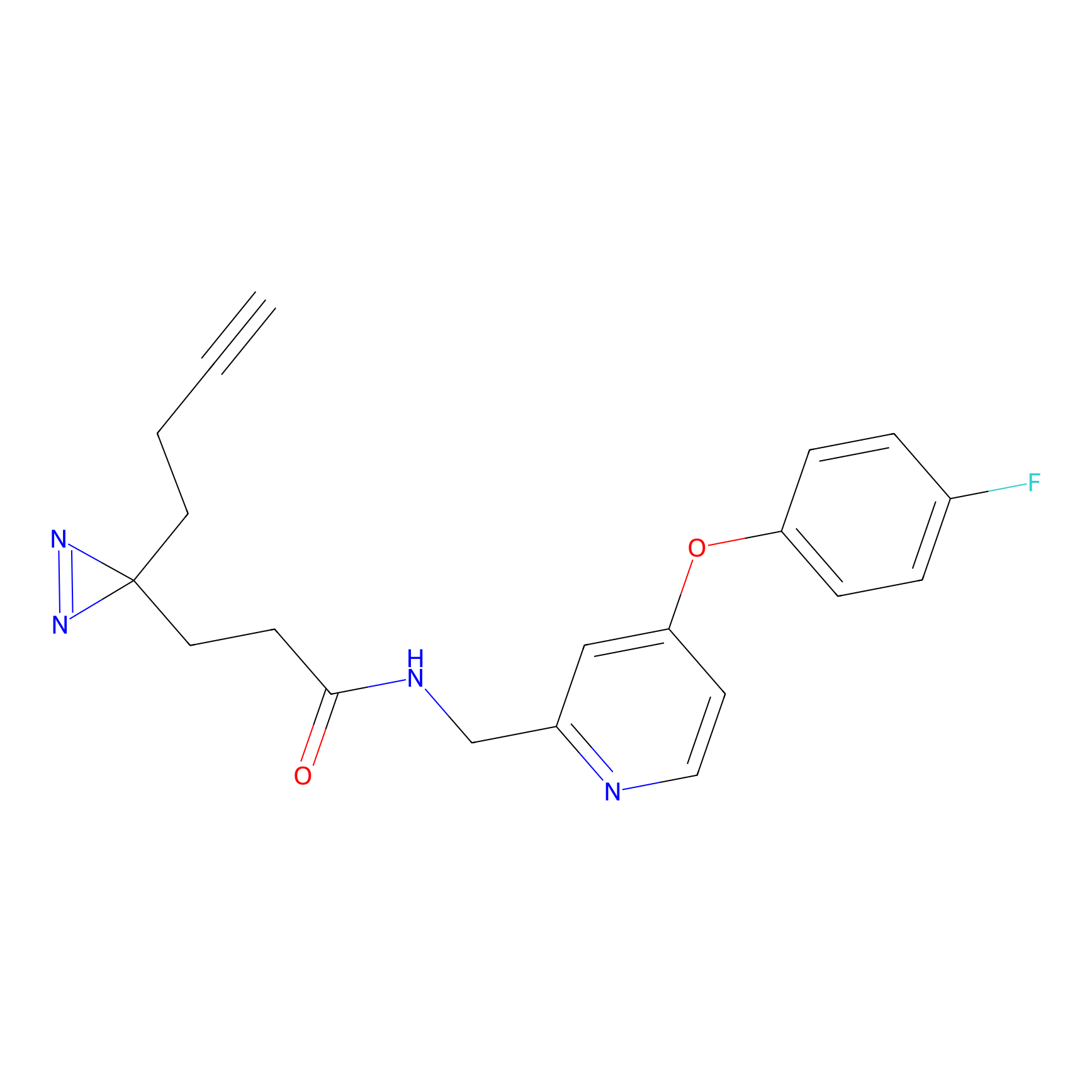
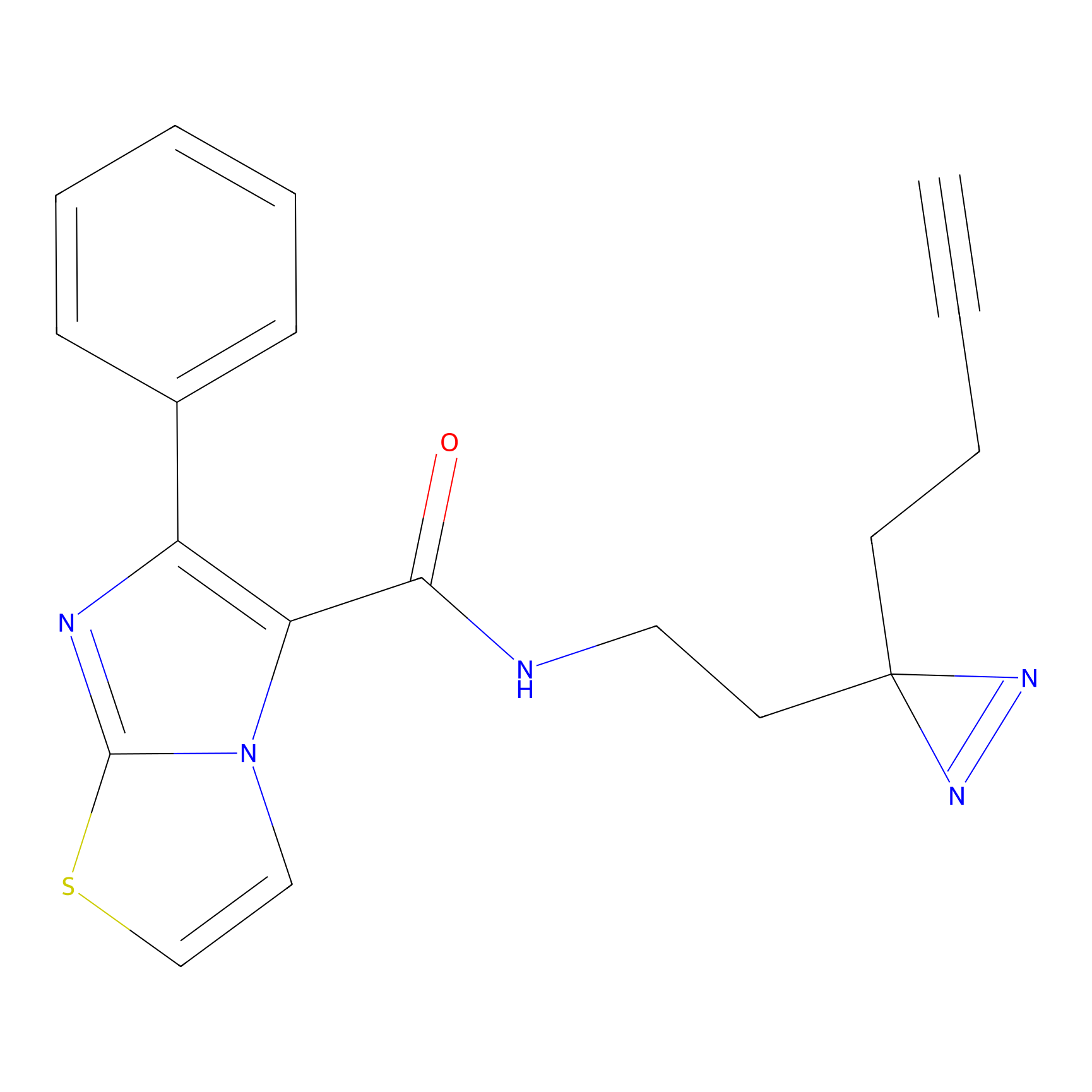
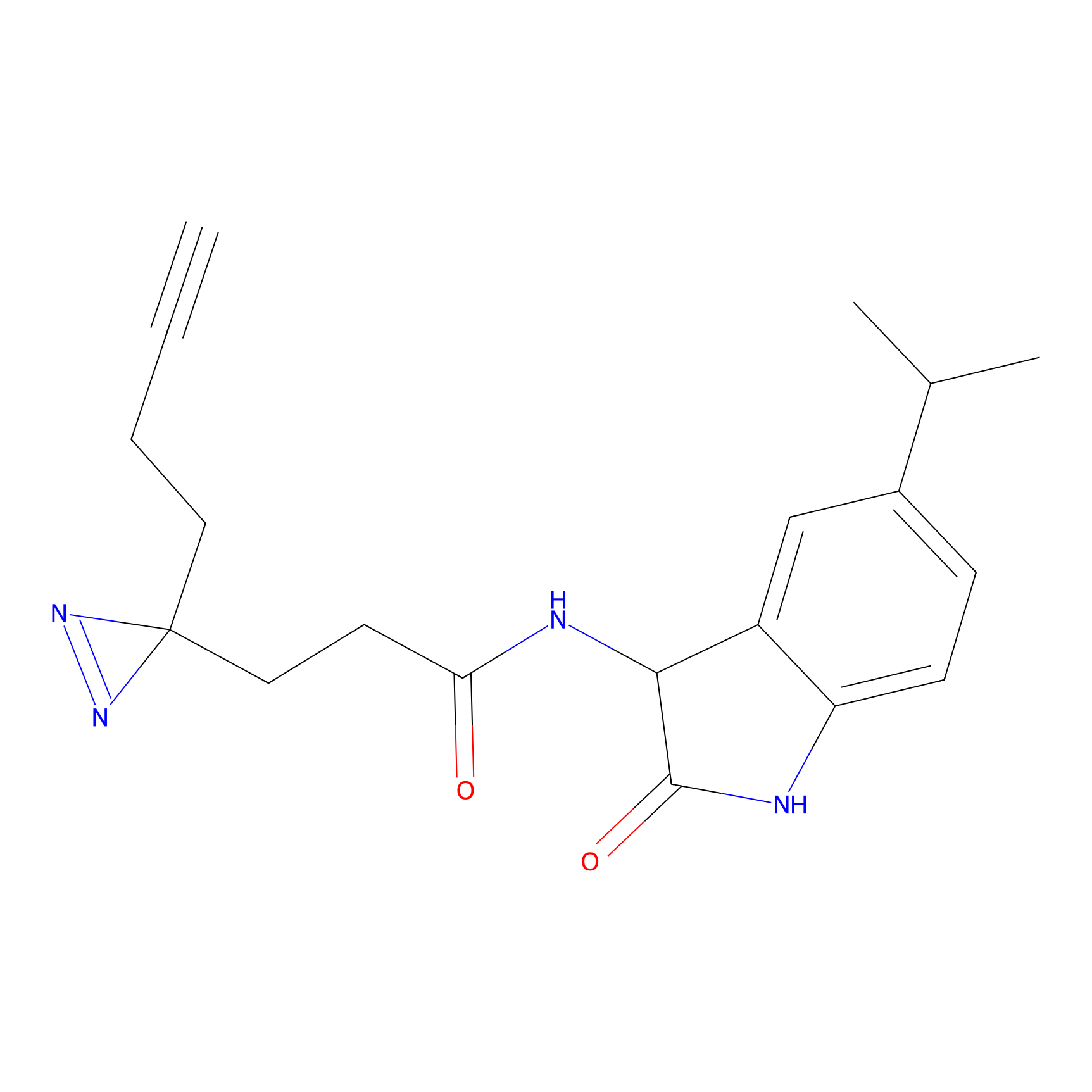
m-APA Probe Info |
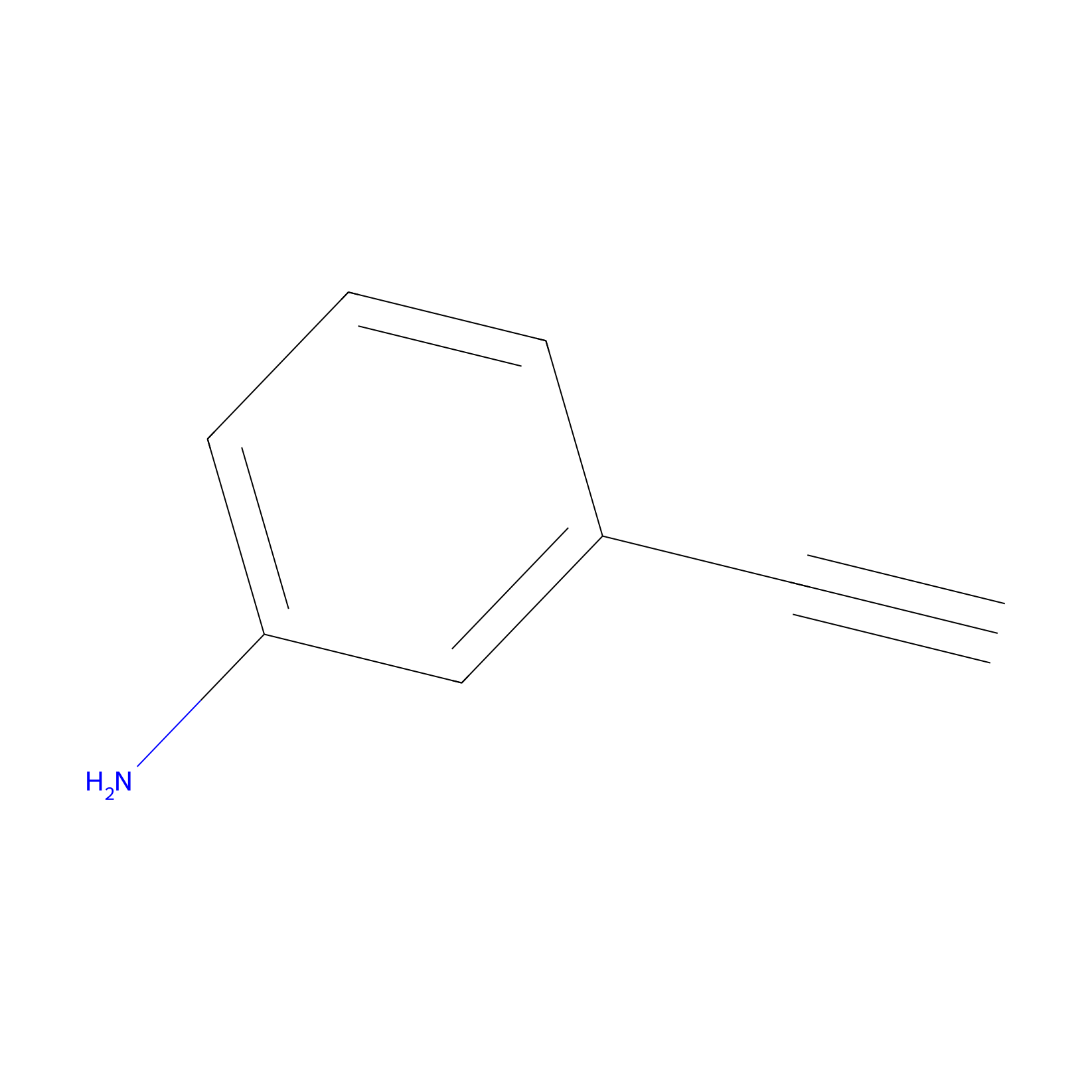 |
N.A. | LDD2231 | [1] | |
PAL-AfBPP Probe
The Interaction Atlas With This Target
References