Details of the Target
General Information of Target
| Target ID | LDTP19780 | |||||
|---|---|---|---|---|---|---|
| Target Name | Keratinocyte-associated transmembrane protein 2 (KCT2) | |||||
| Gene Name | KCT2 | |||||
| Gene ID | 56951 | |||||
| Synonyms |
C5orf15; Keratinocyte-associated transmembrane protein 2 |
|||||
| 3D Structure | ||||||
| Sequence |
MLAVPVRLKVGSRKPEWGTNRLTSCPAKDPLDRRLQNLRDRERVPEPQRSLRPGVQEDSR
EHGQVPEVSDPQVDLEFVDLQAKPRYRRLILKTQIPEASDSQAAQKPQAHRQIPETTEAG RETTSN |
|||||
| Target Bioclass |
Other
|
|||||
| Subcellular location |
Membrane
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Probe(s) Labeling This Target
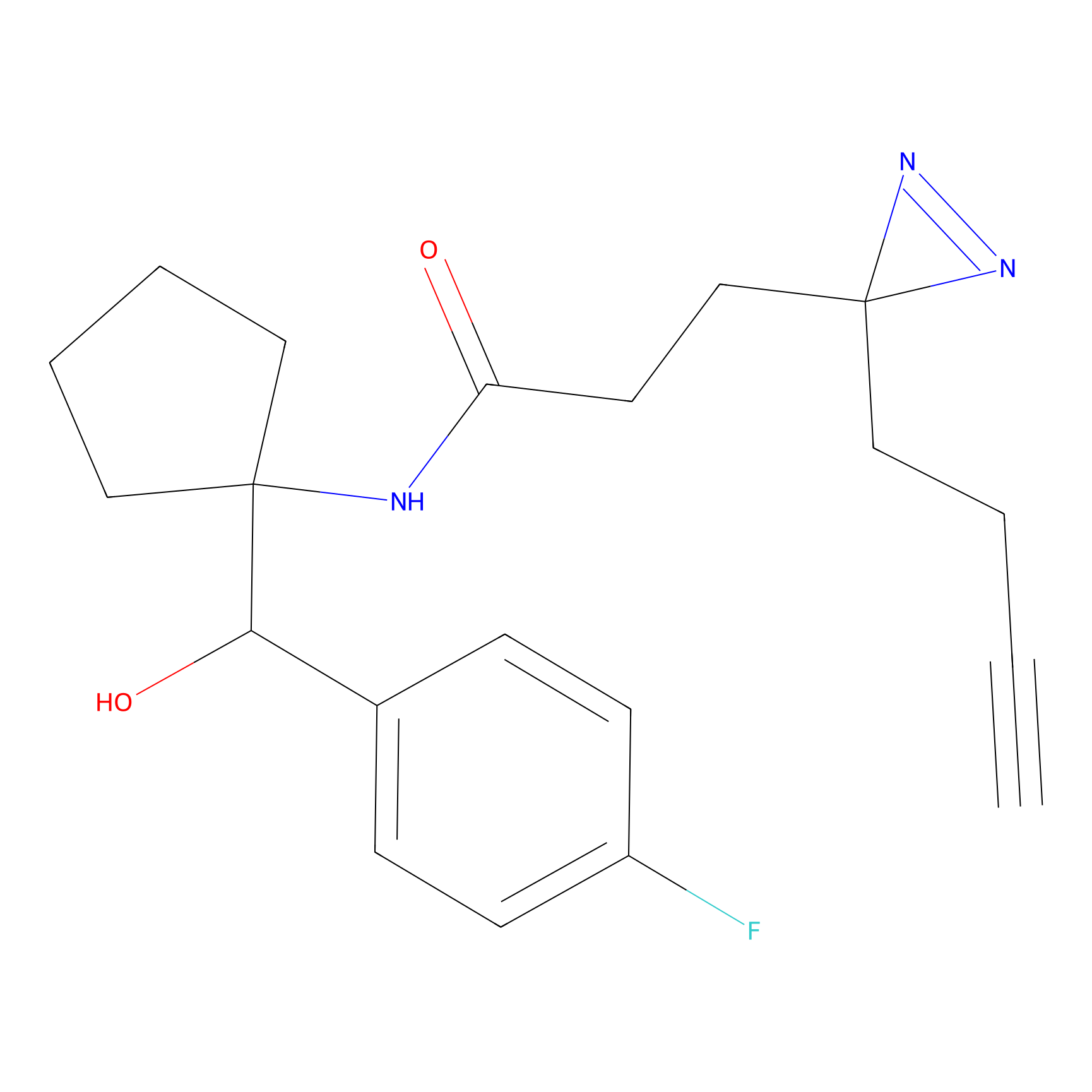
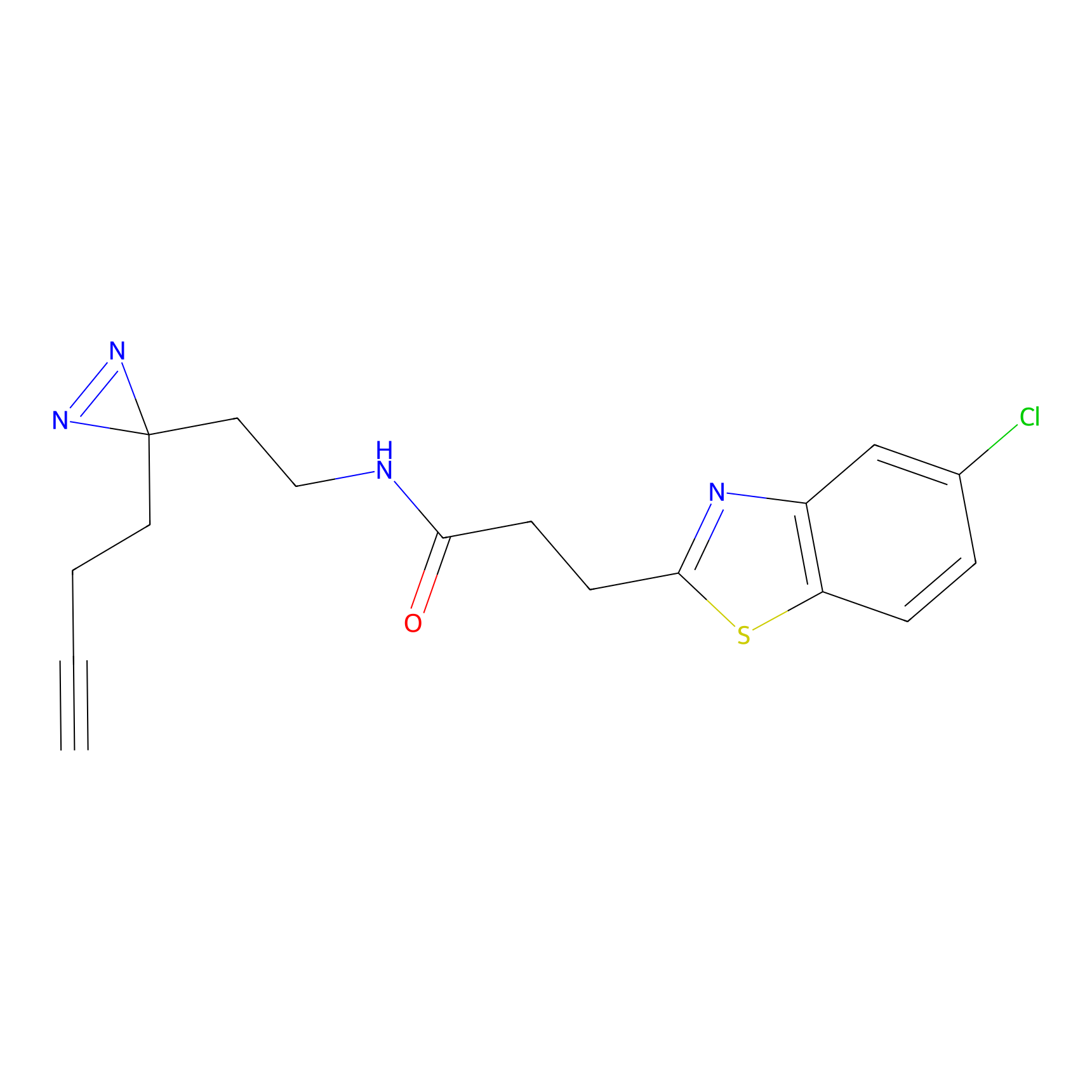
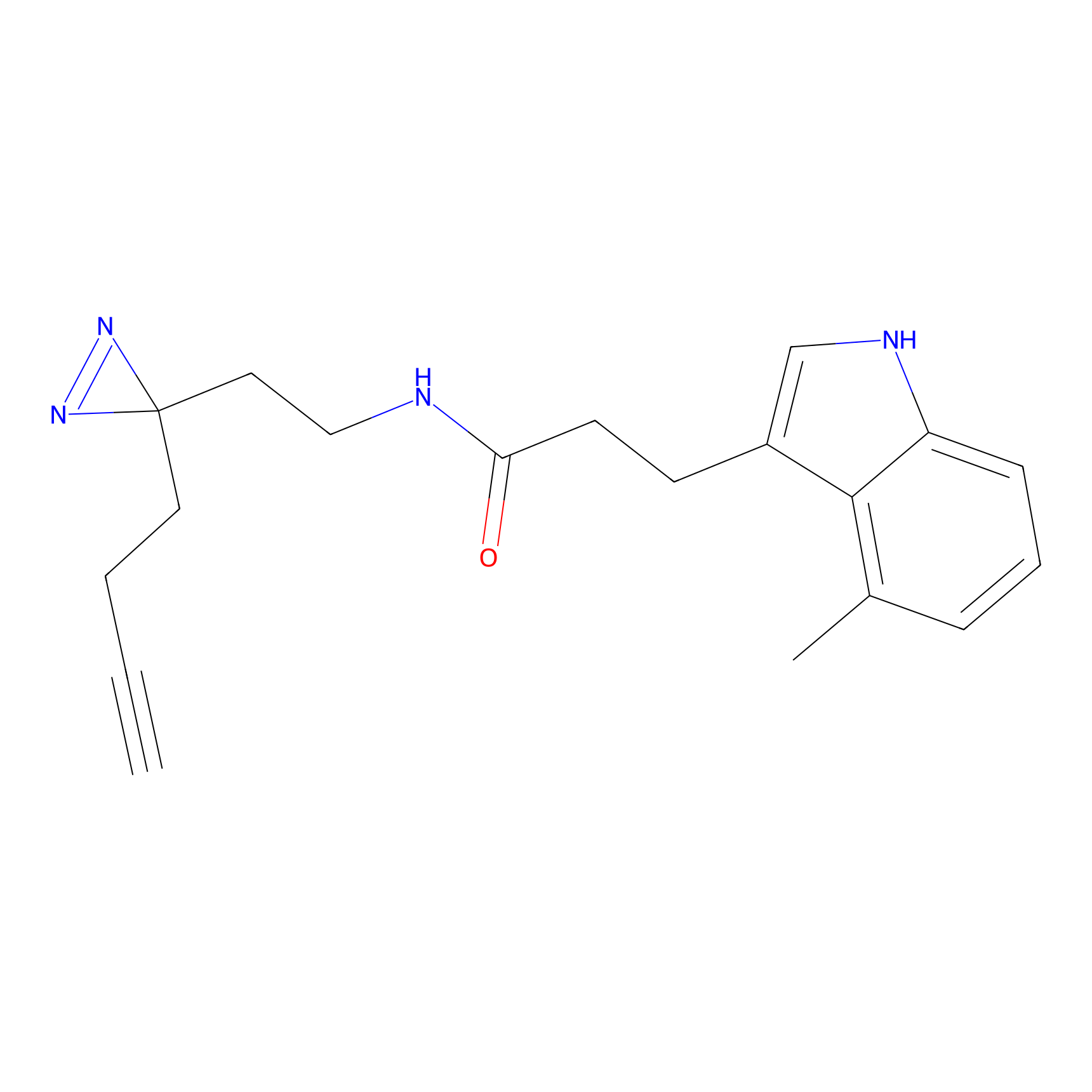
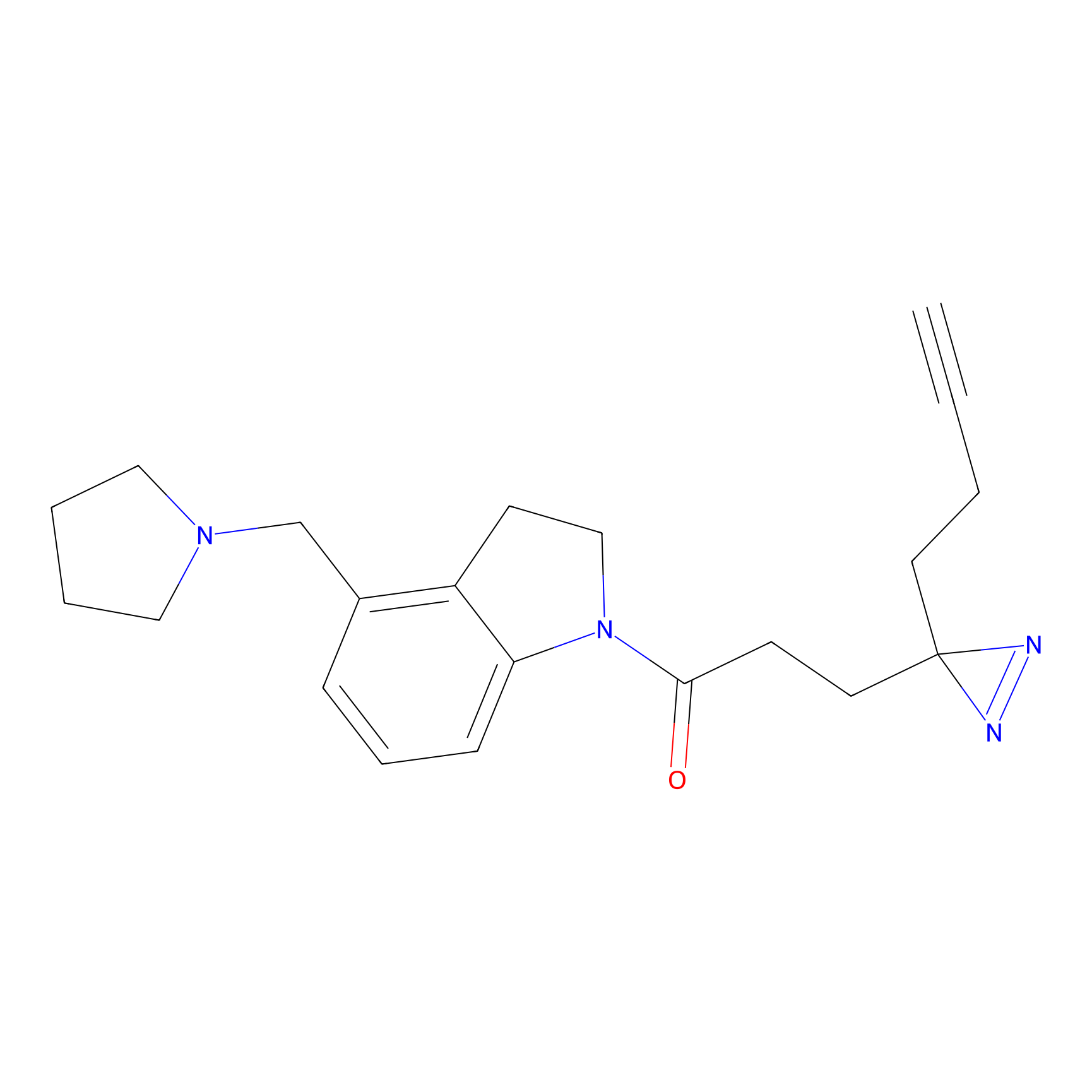
ABPP Probe
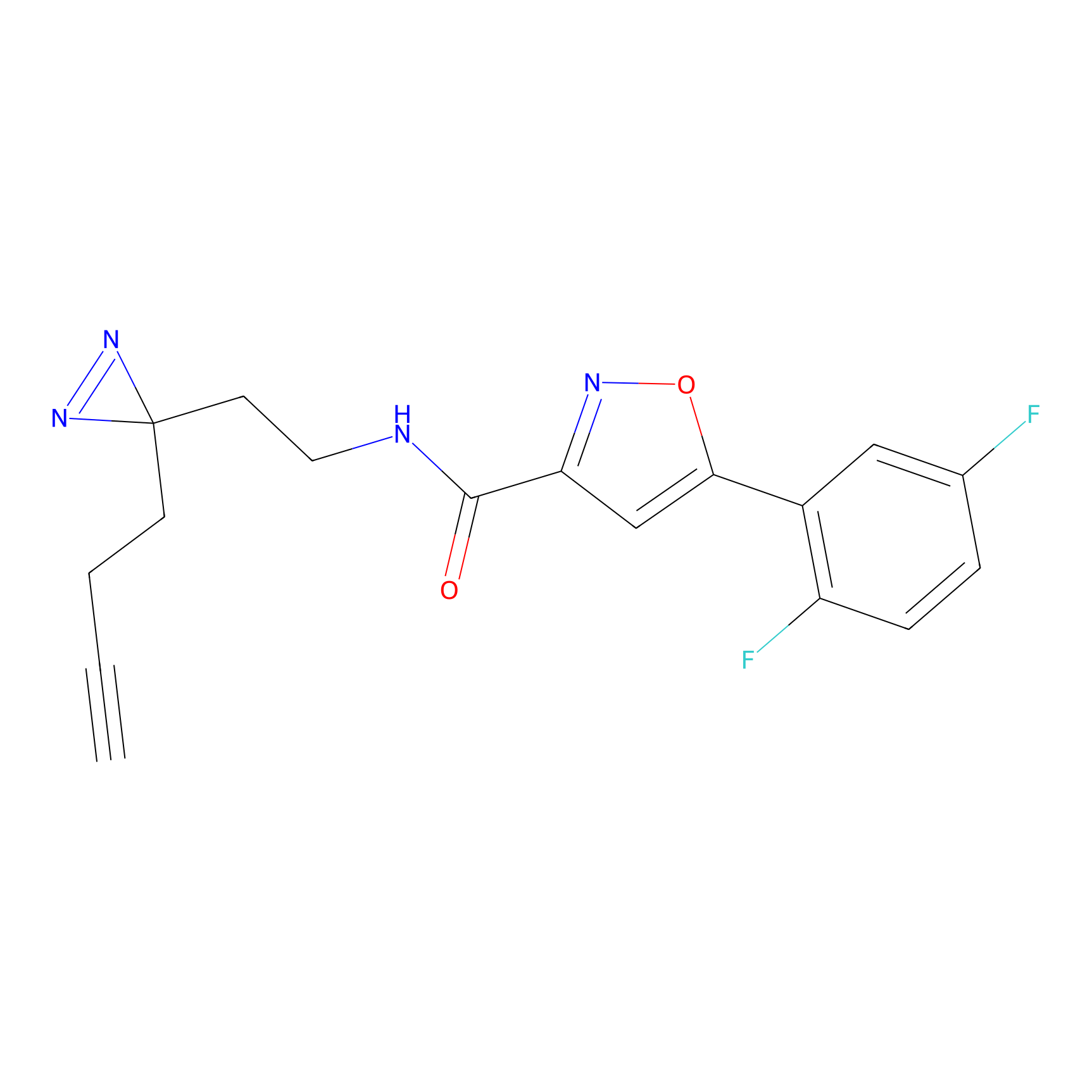
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
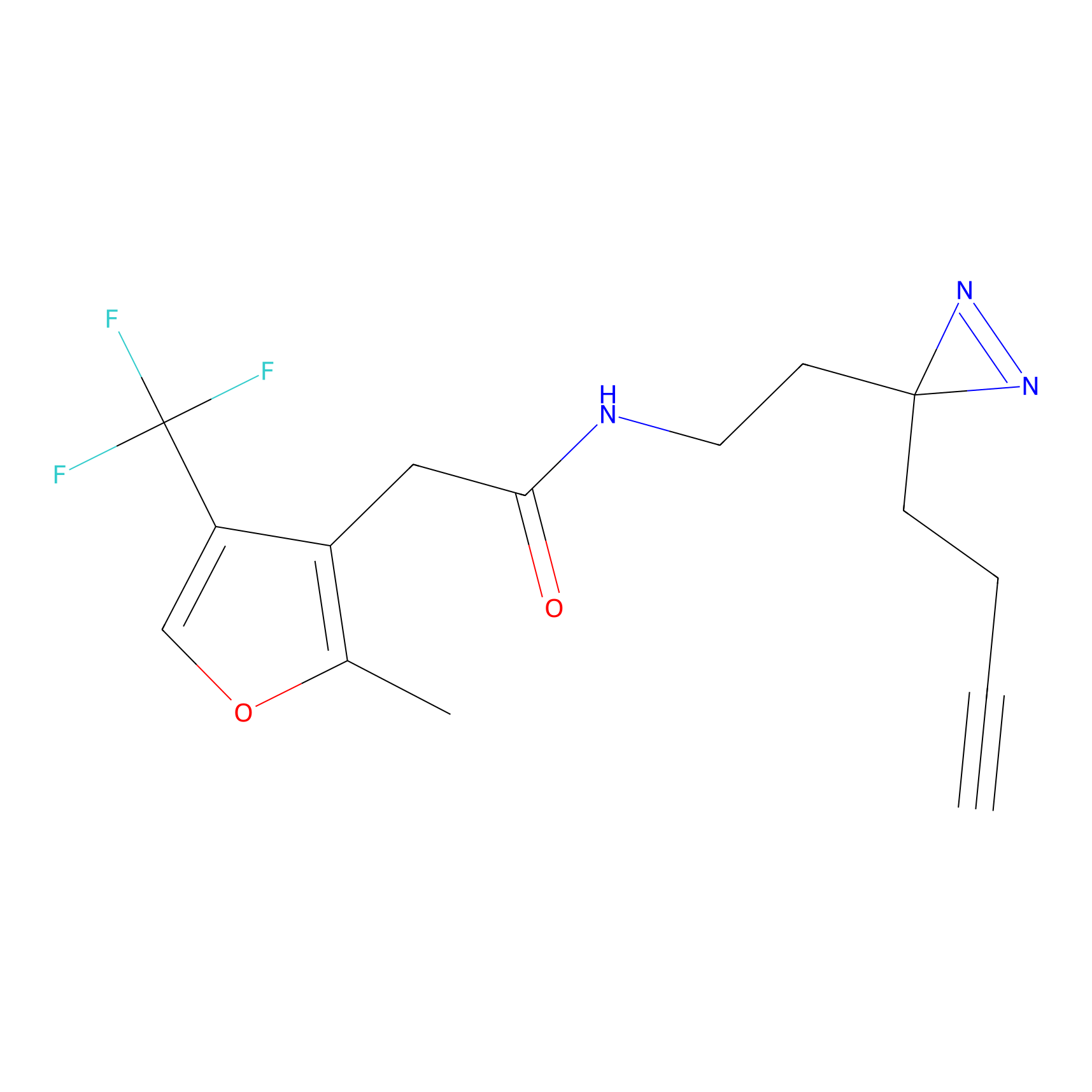
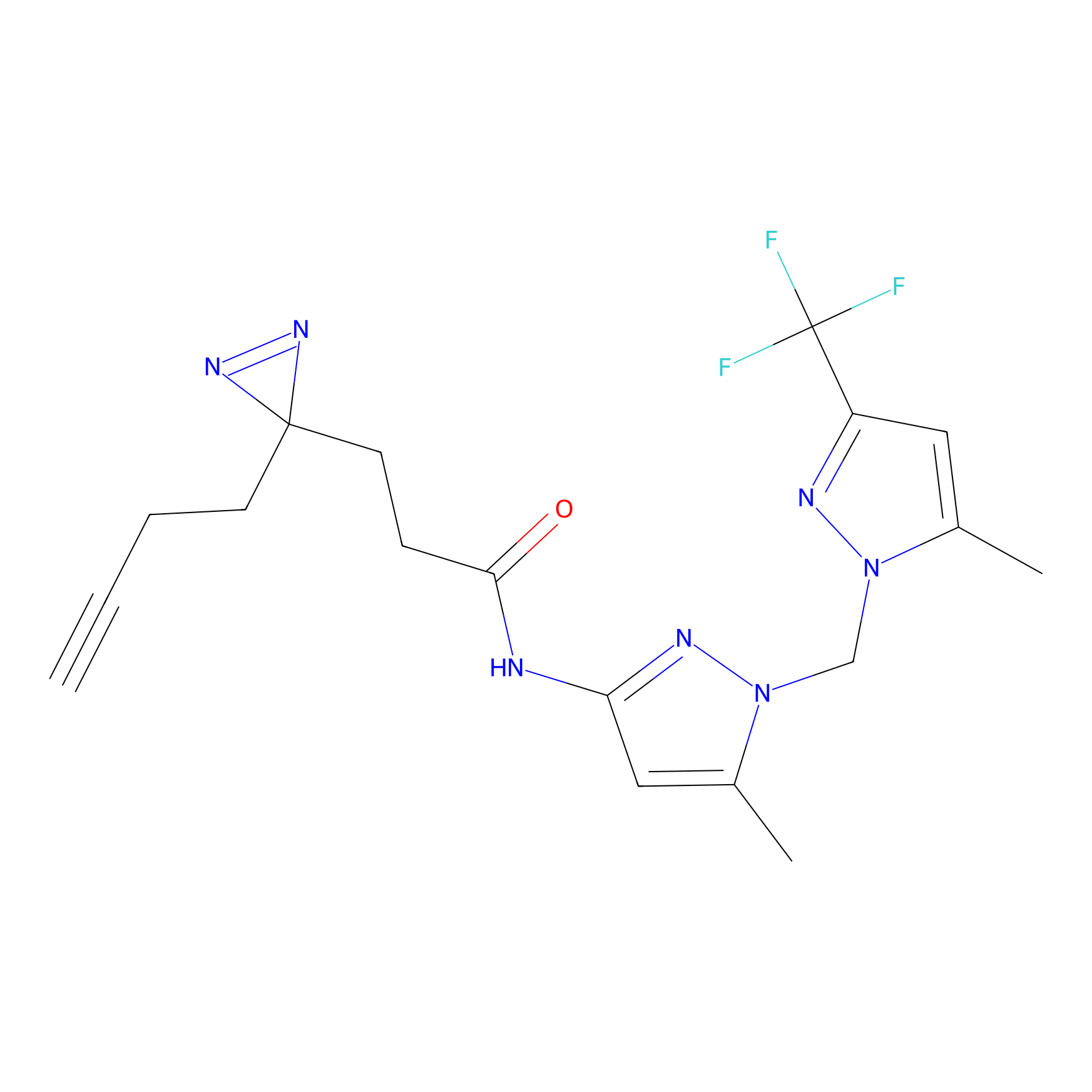
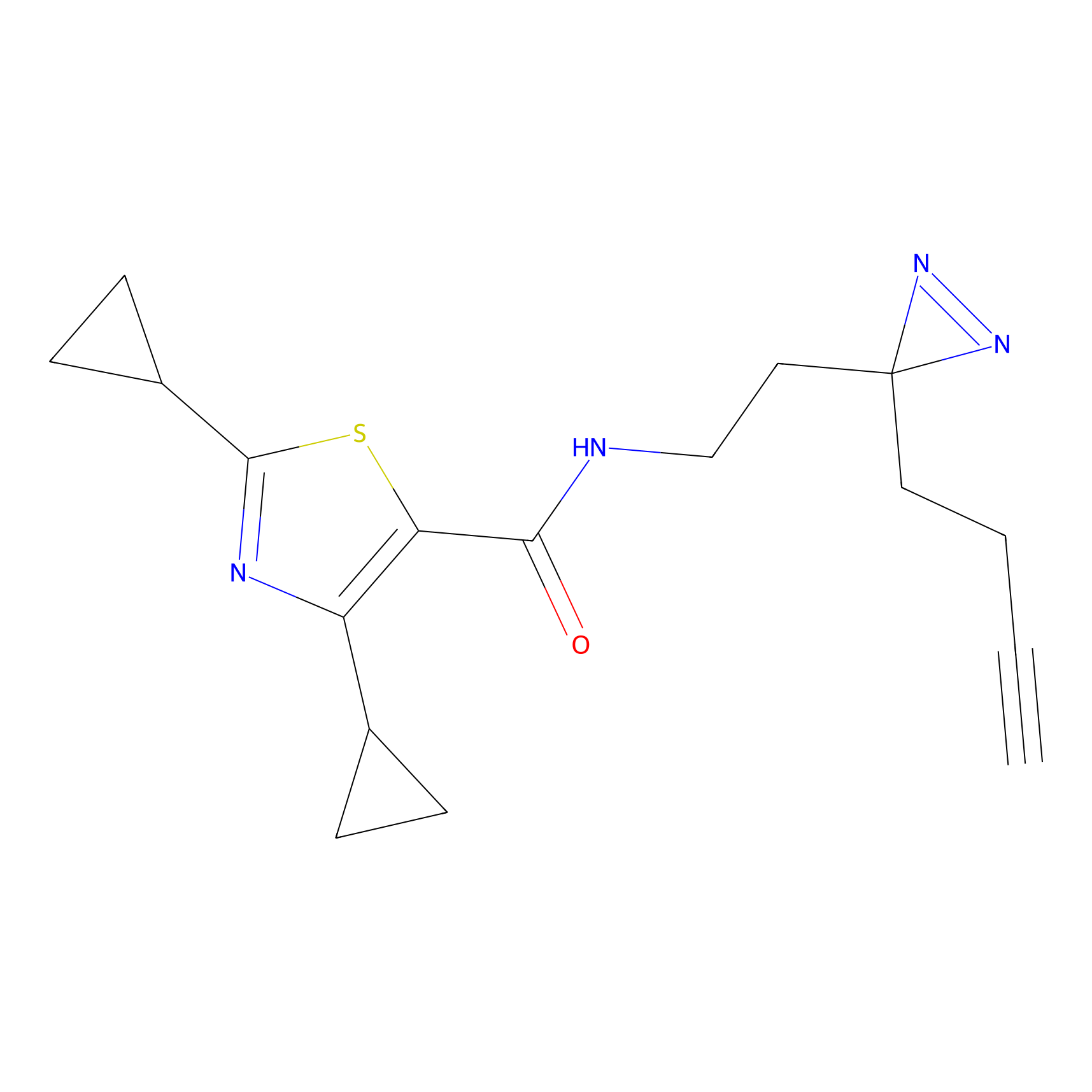
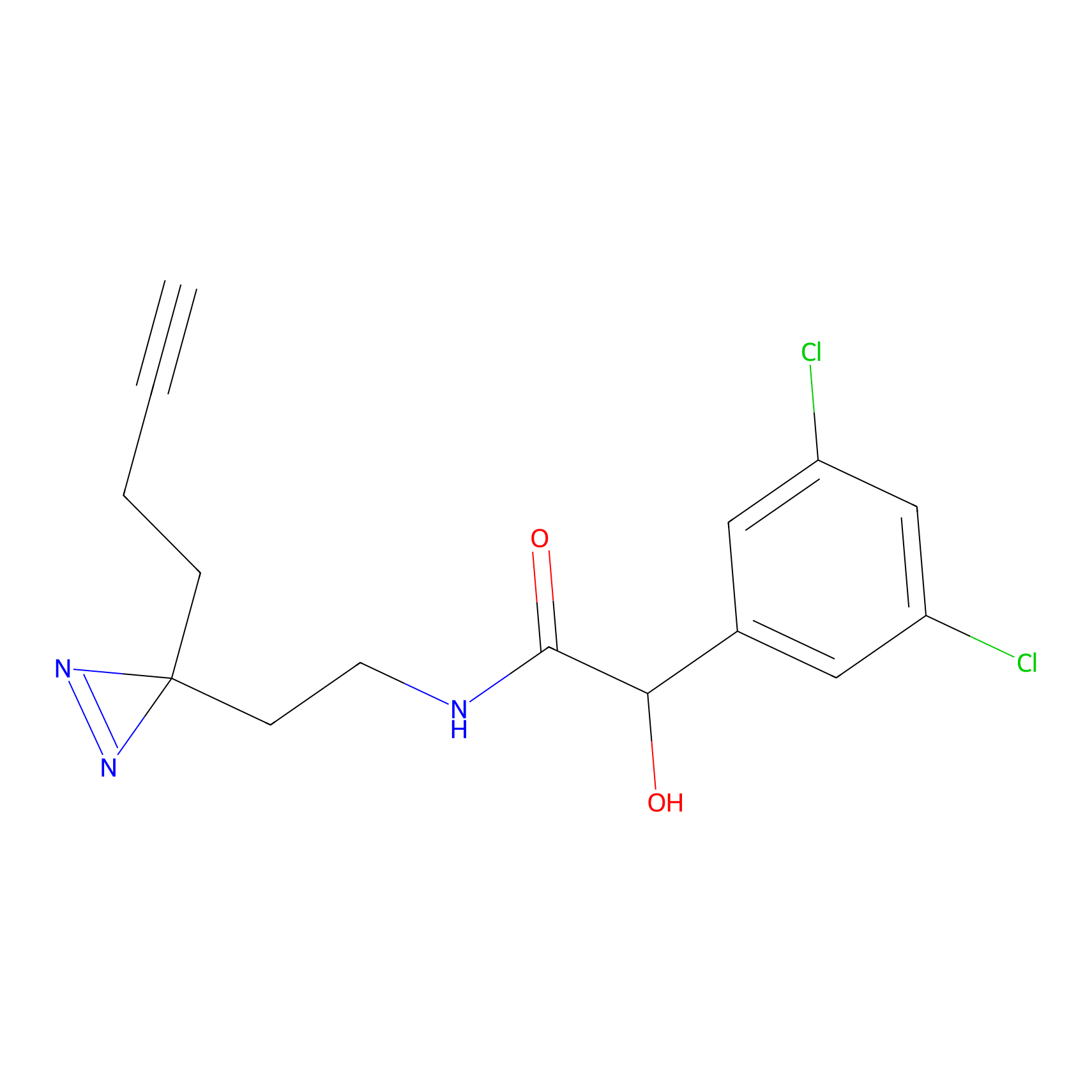
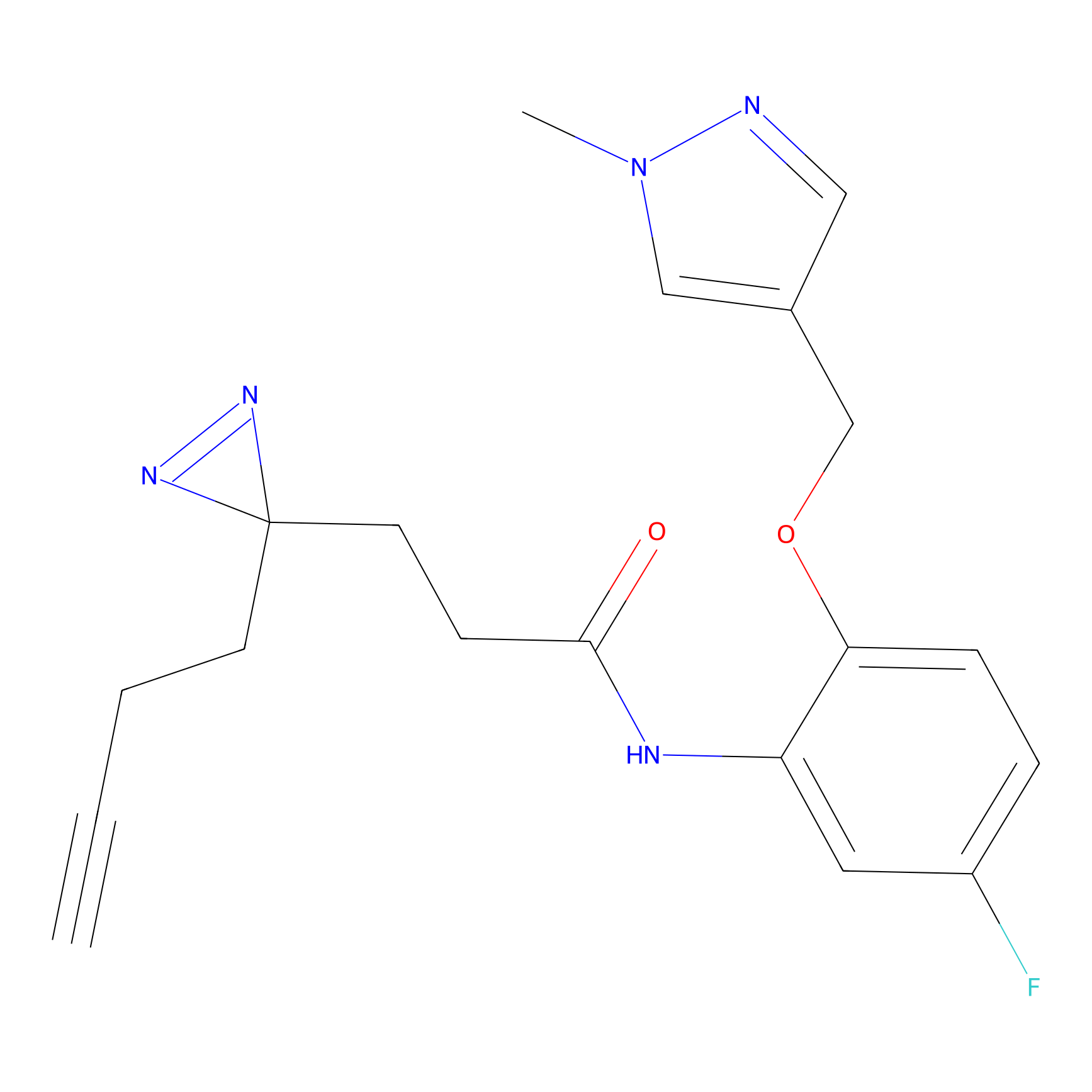
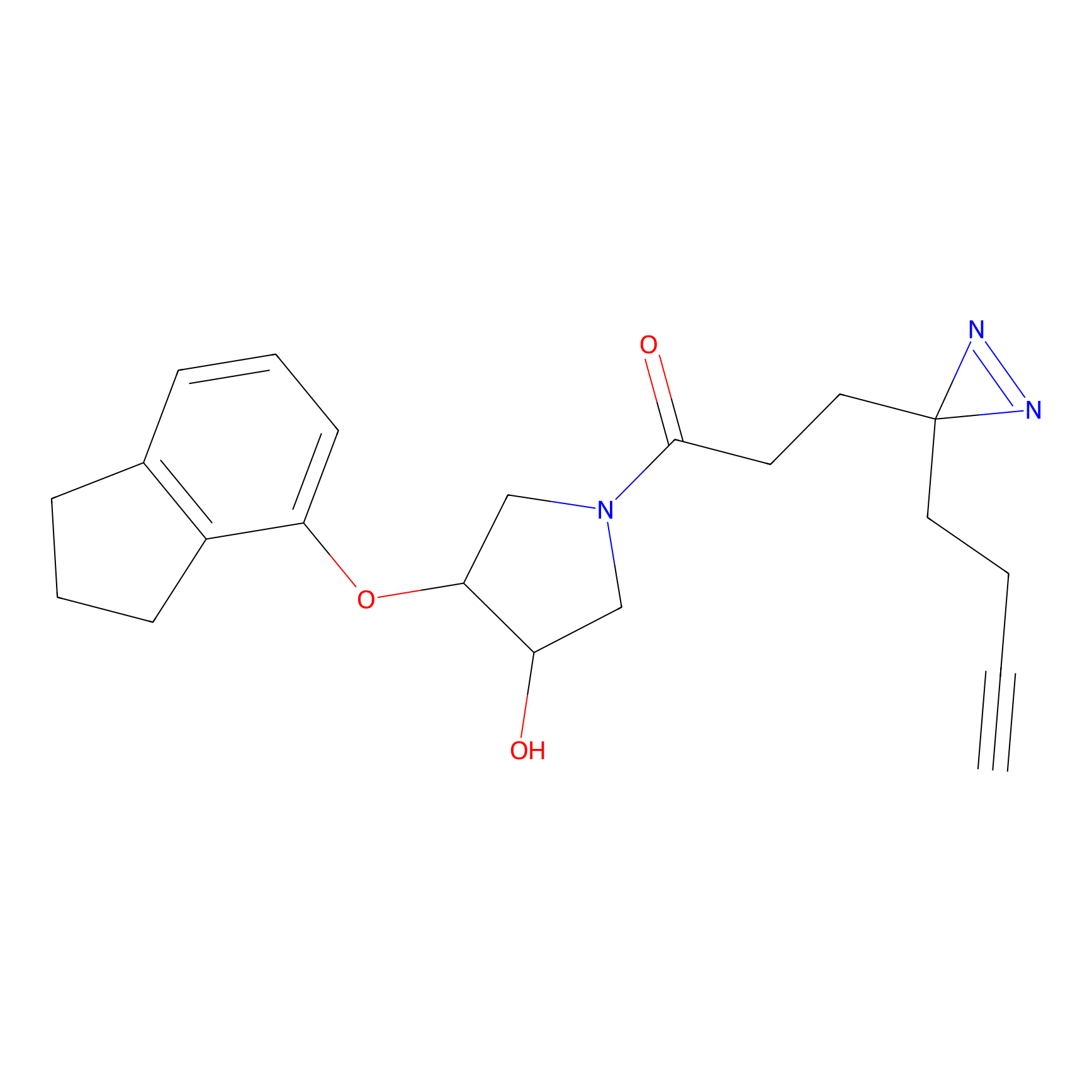
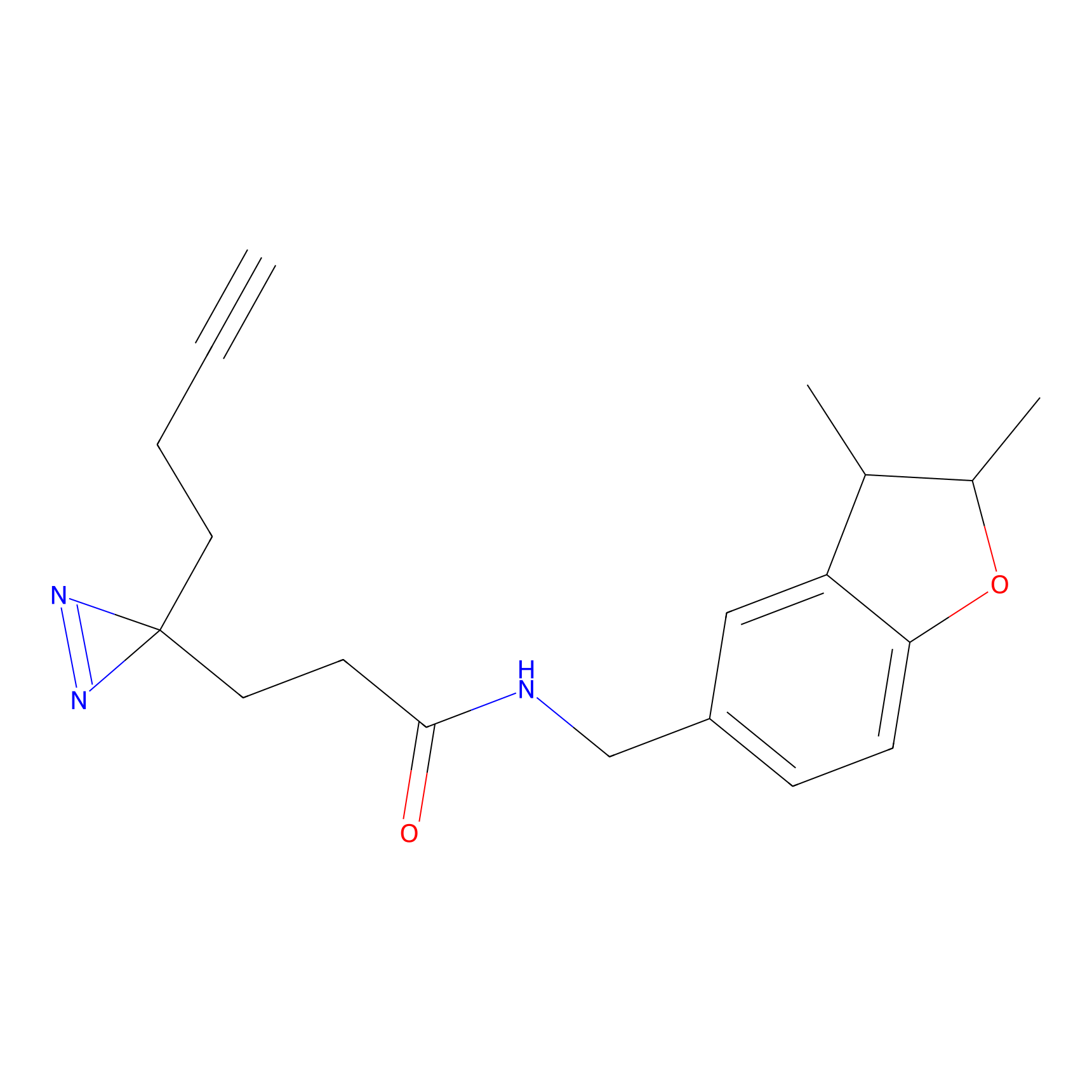
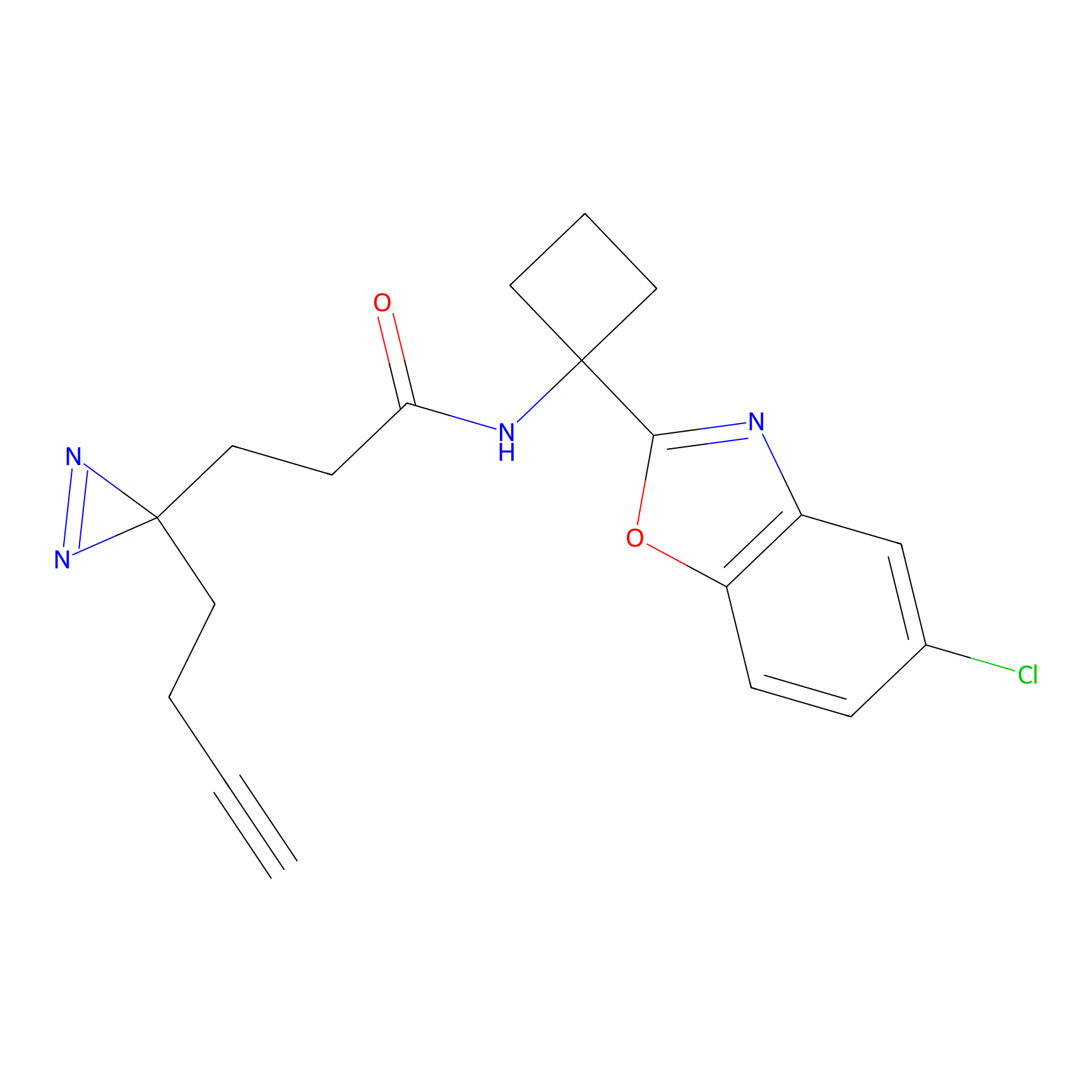
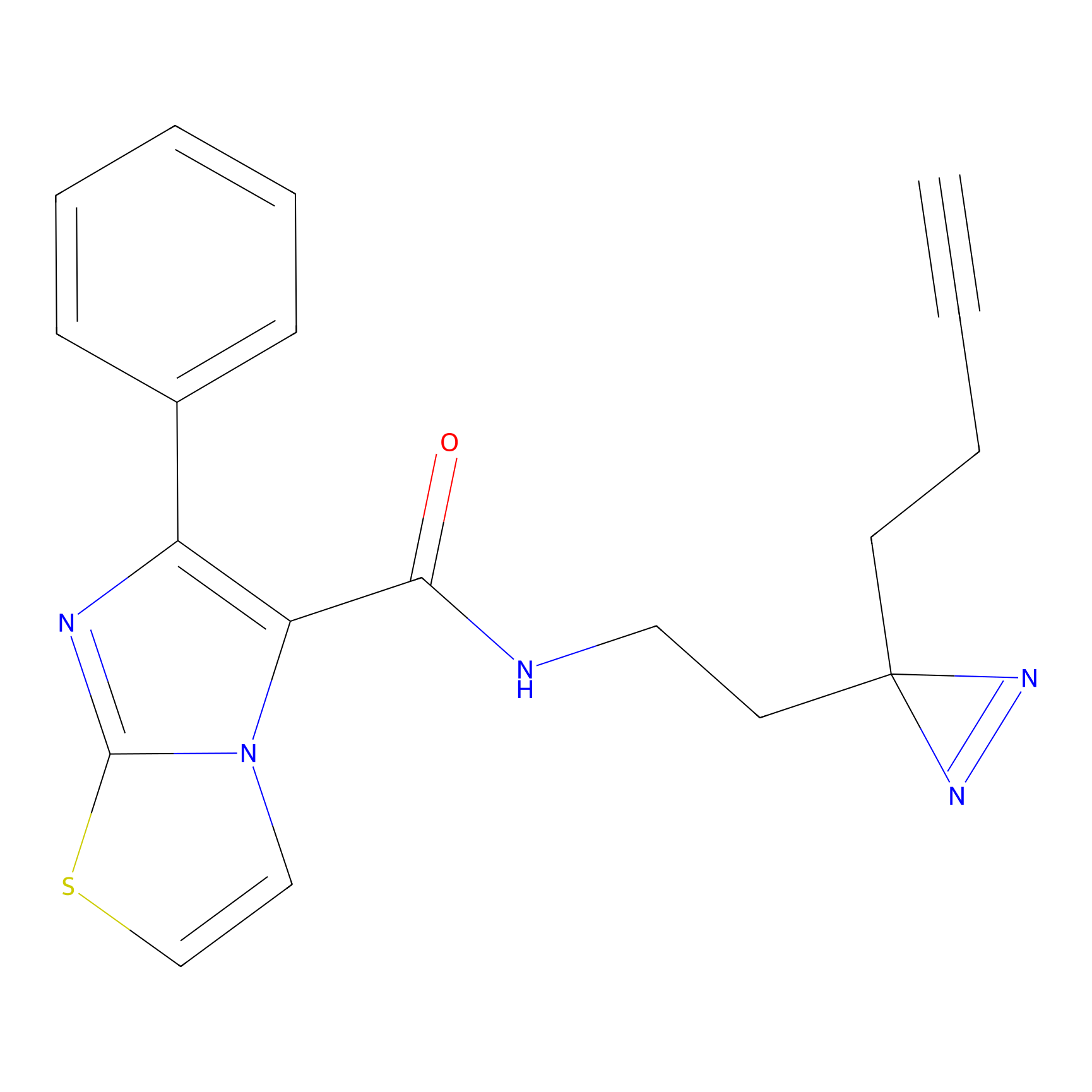
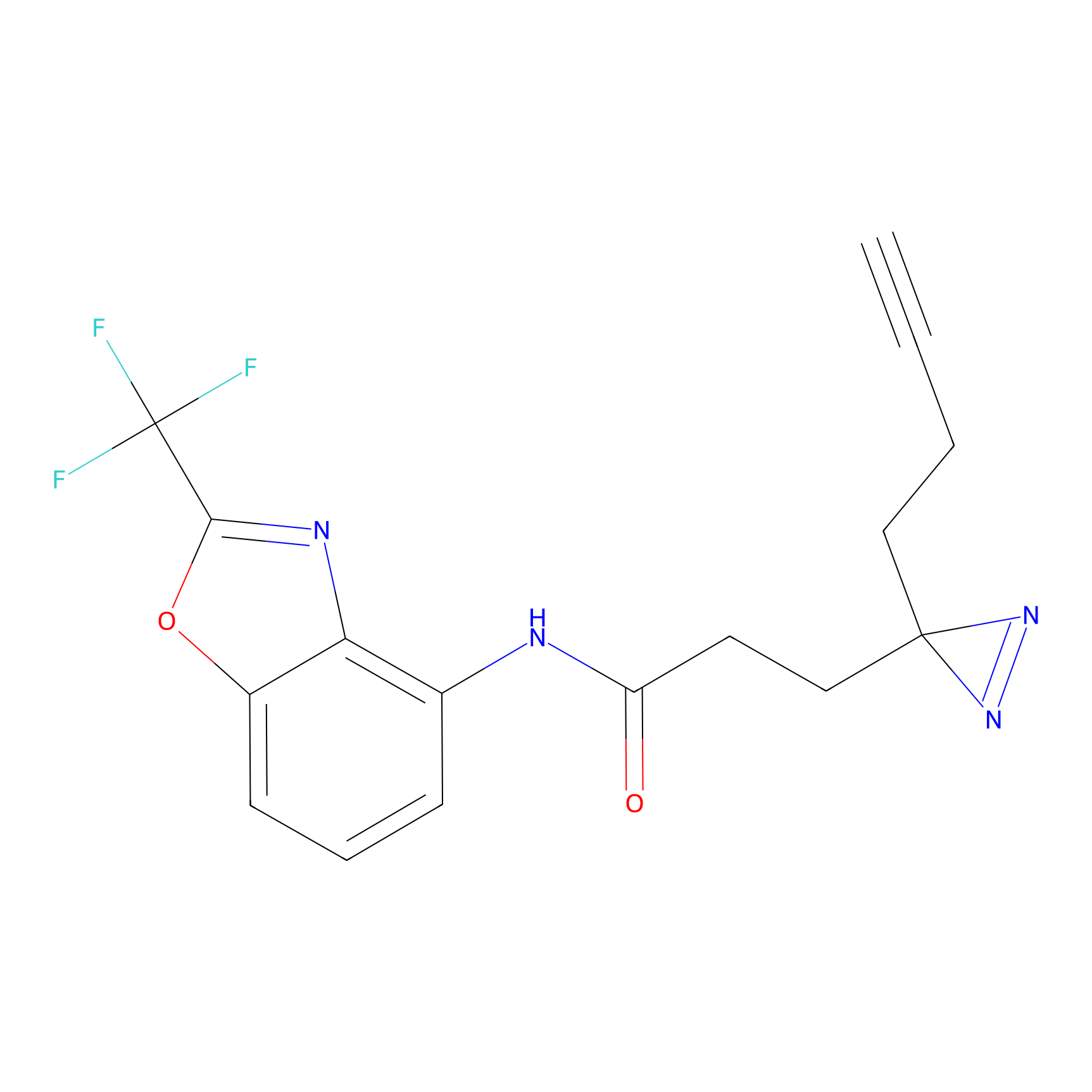
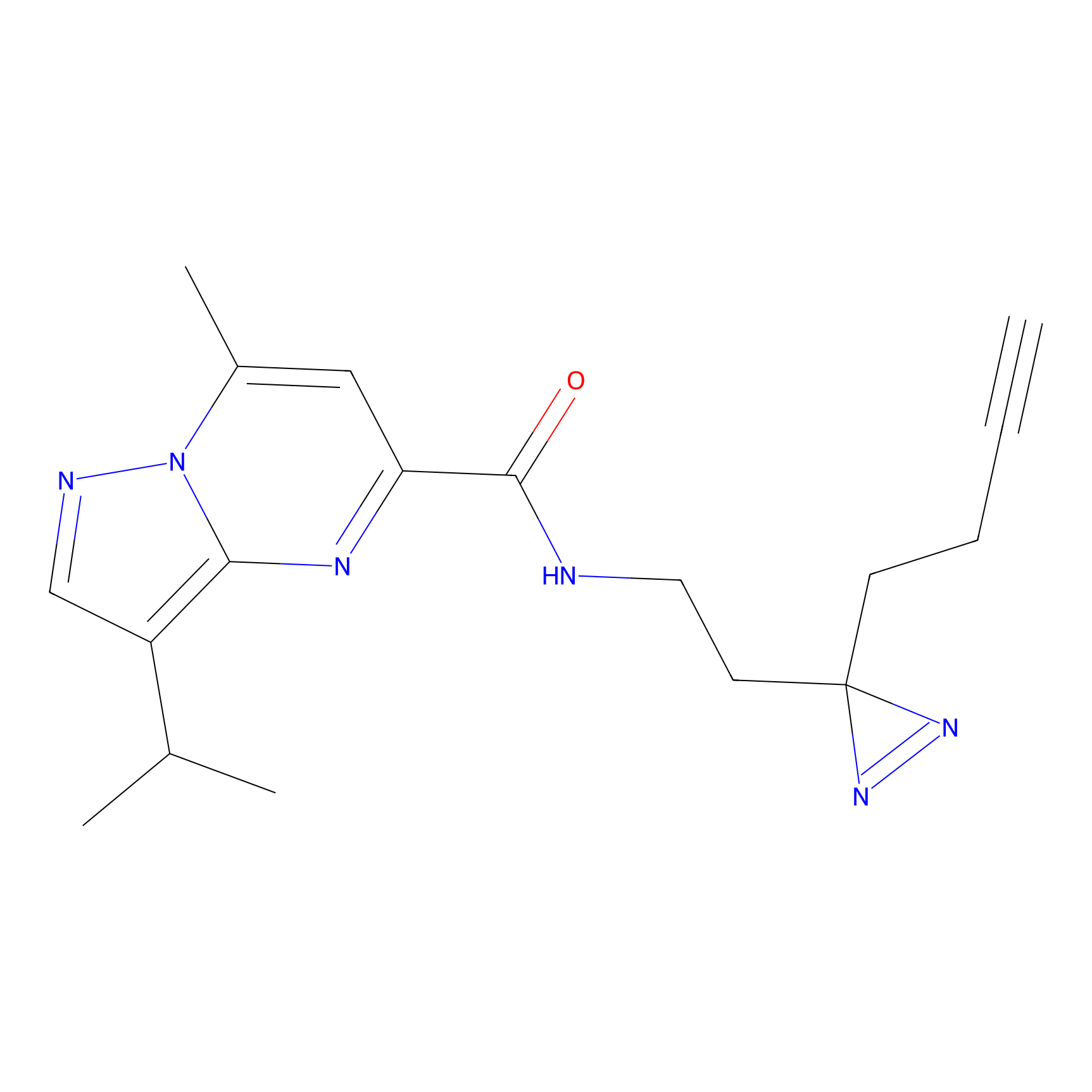
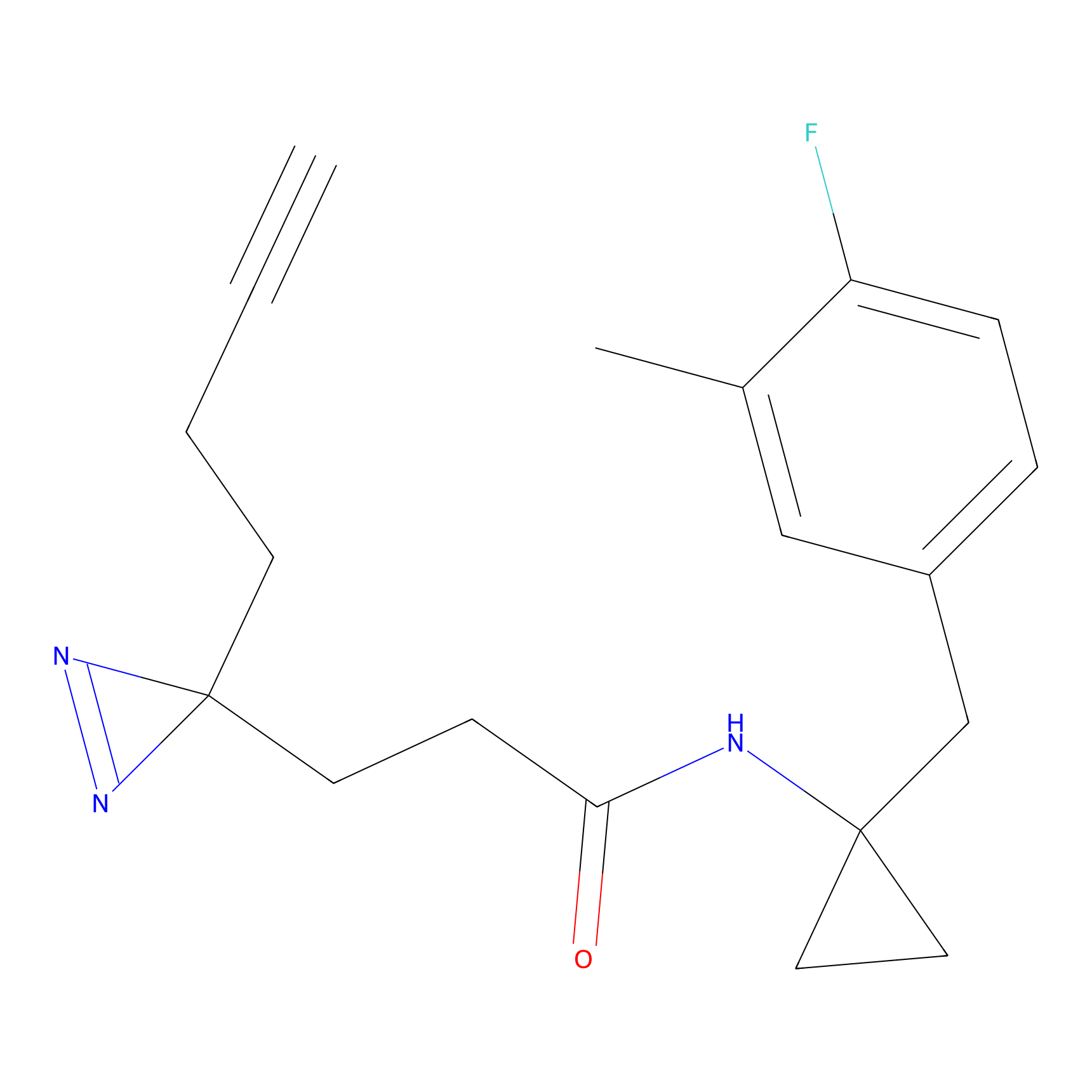
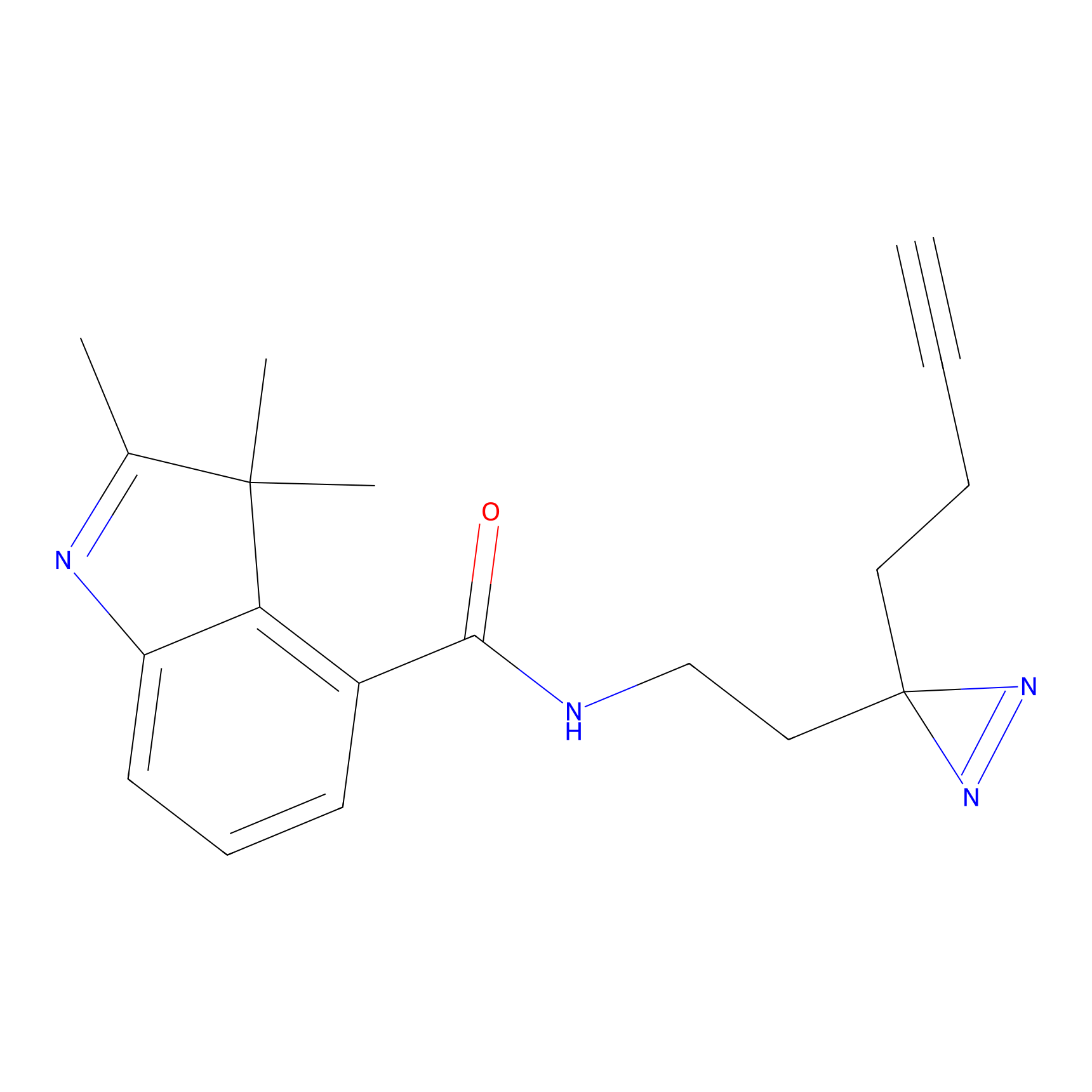
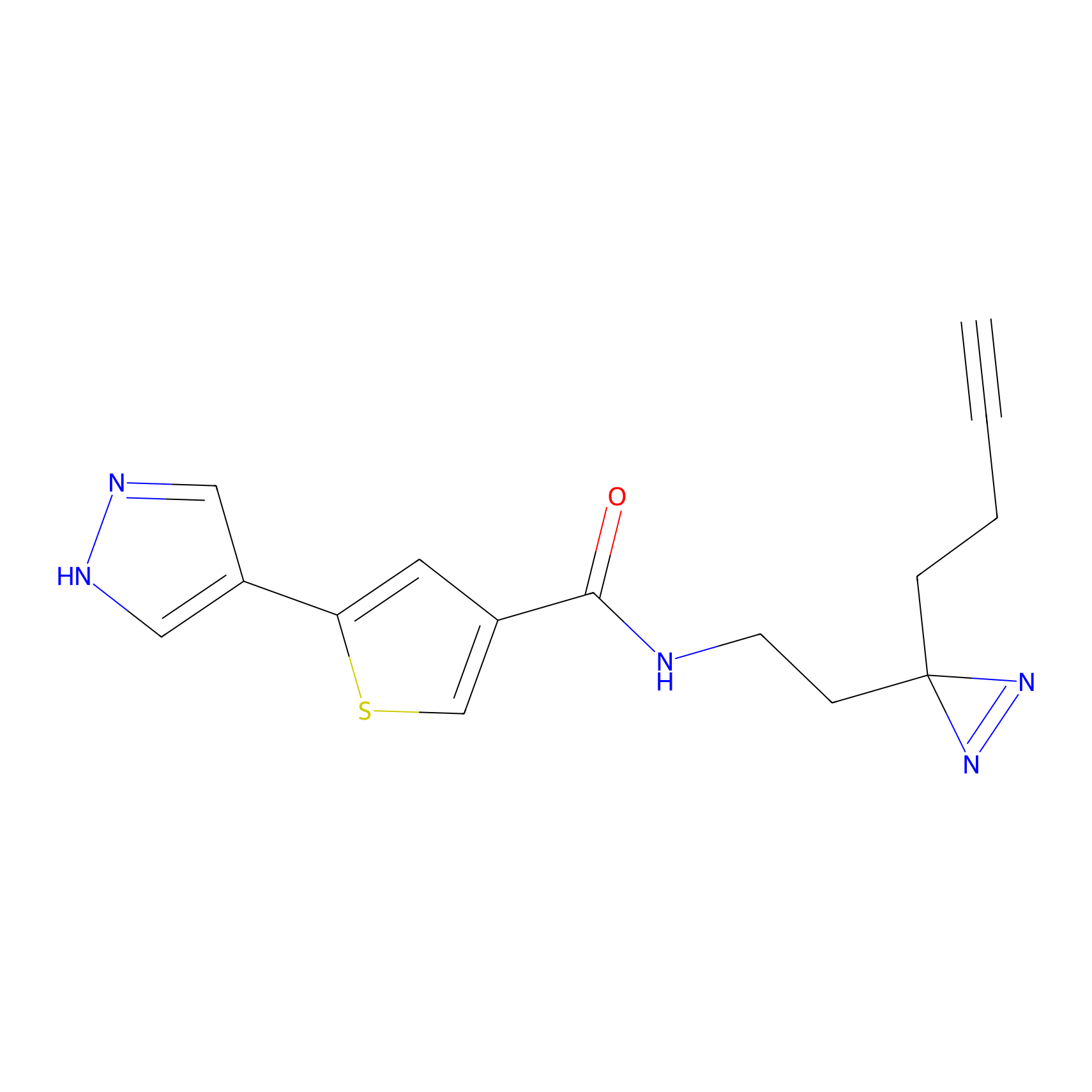
|
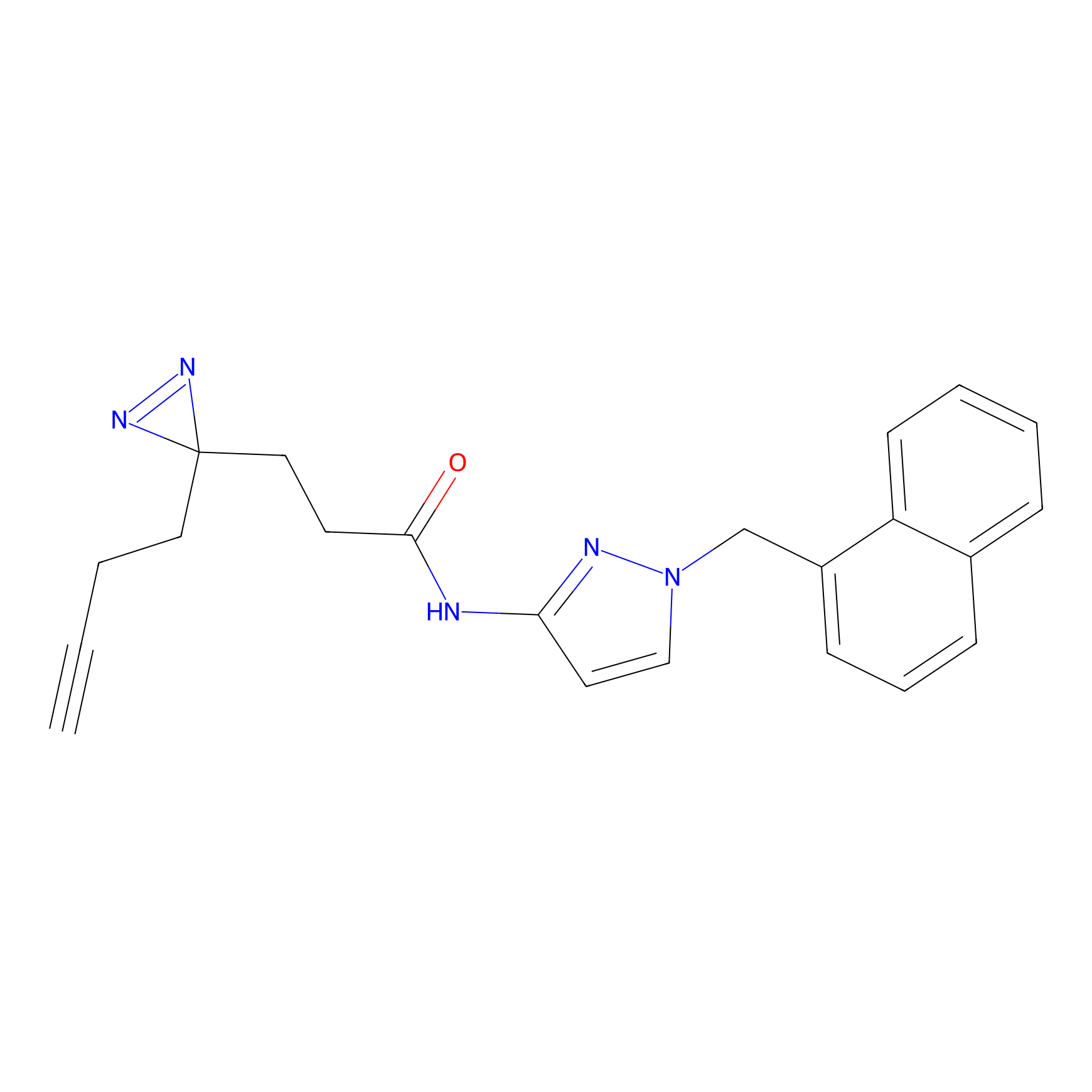
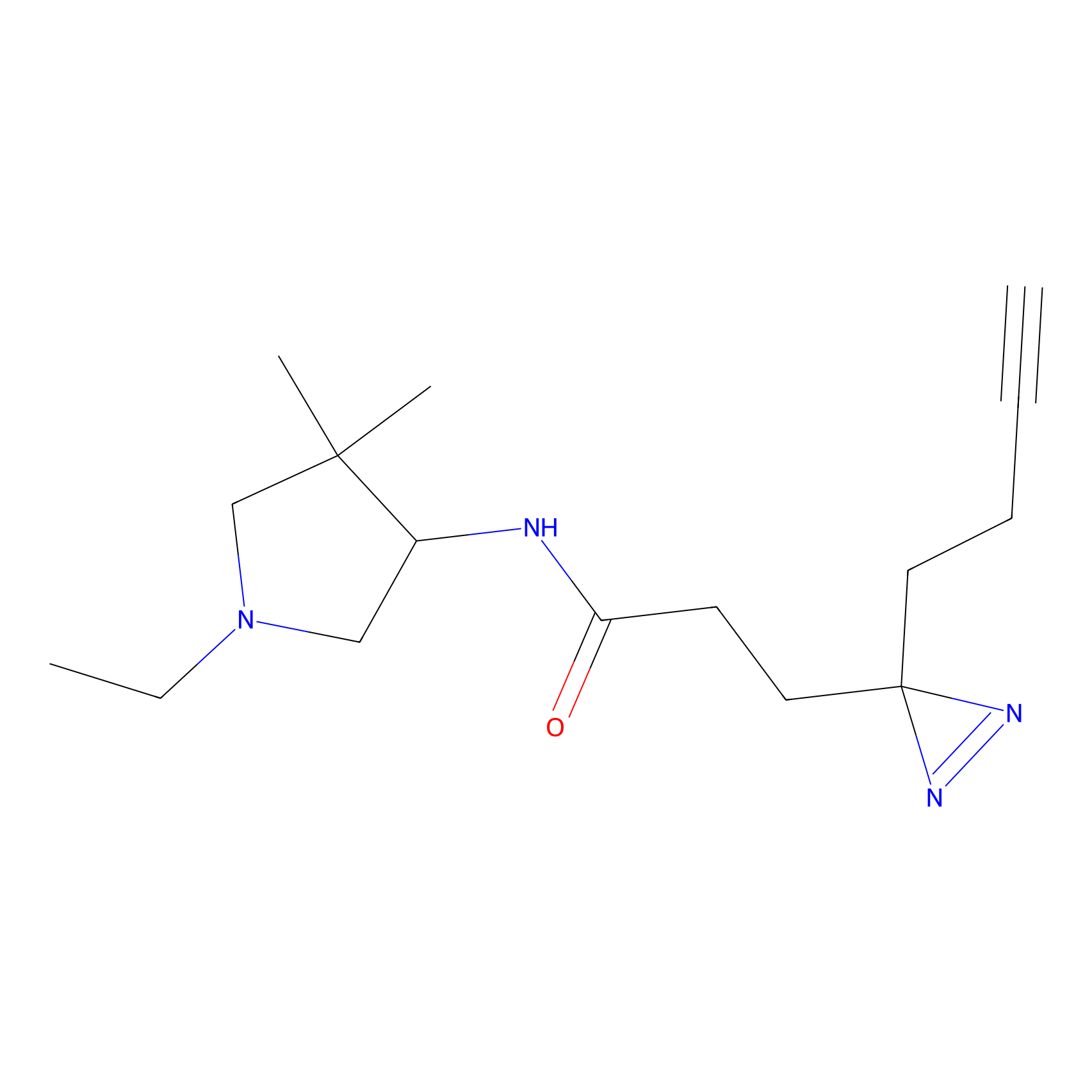
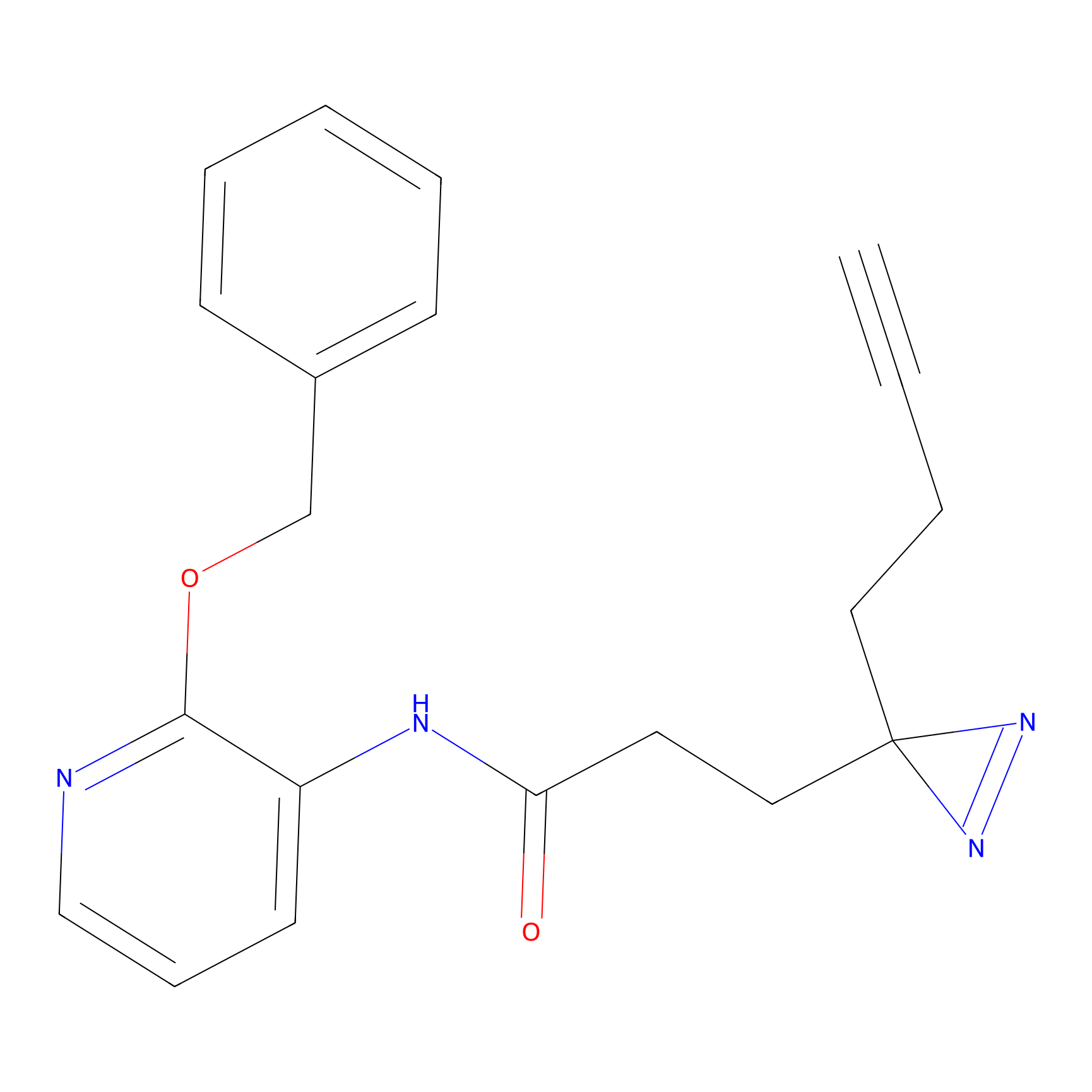
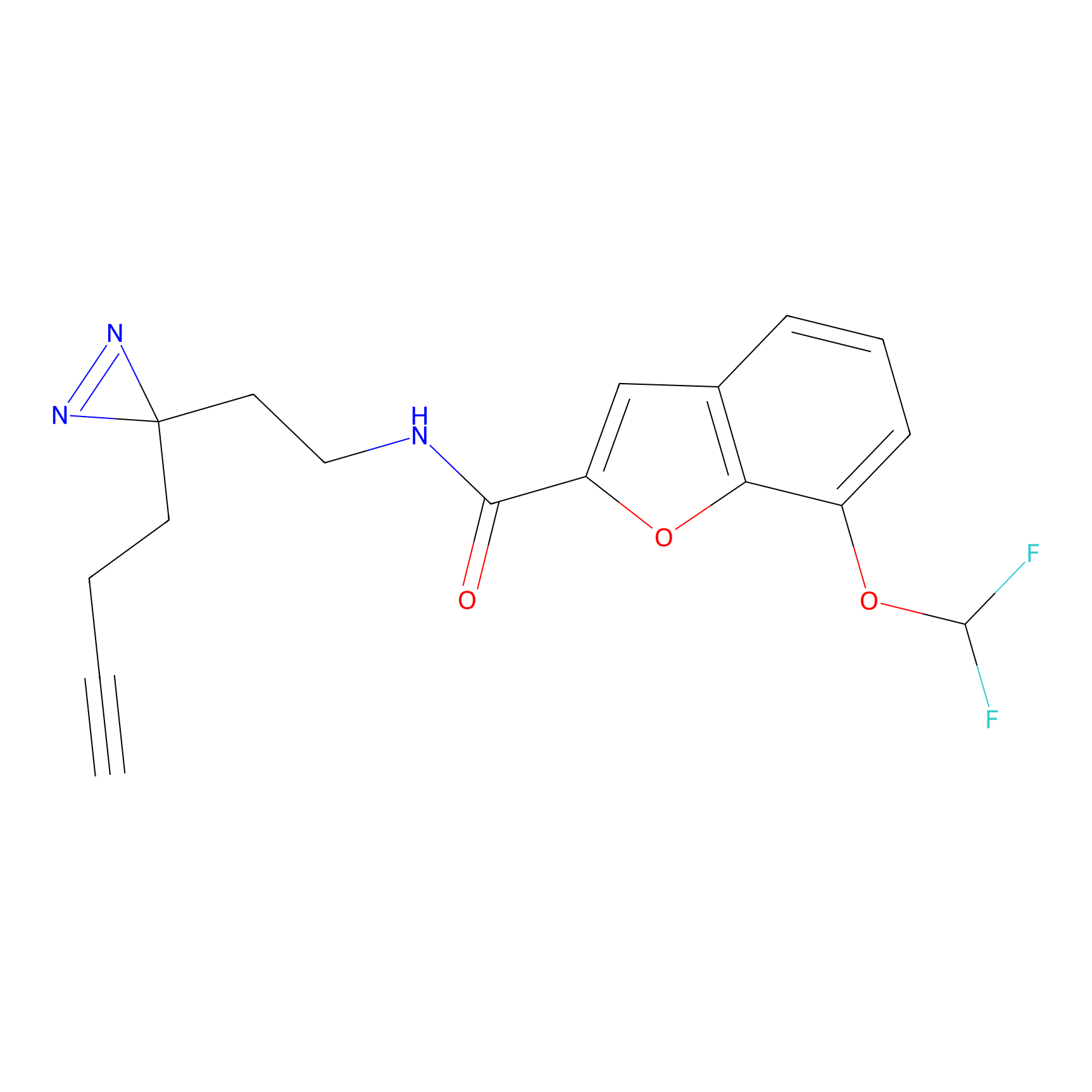
FBPP2 Probe Info |
 |
20.12 | LDD0318 | [1] | |
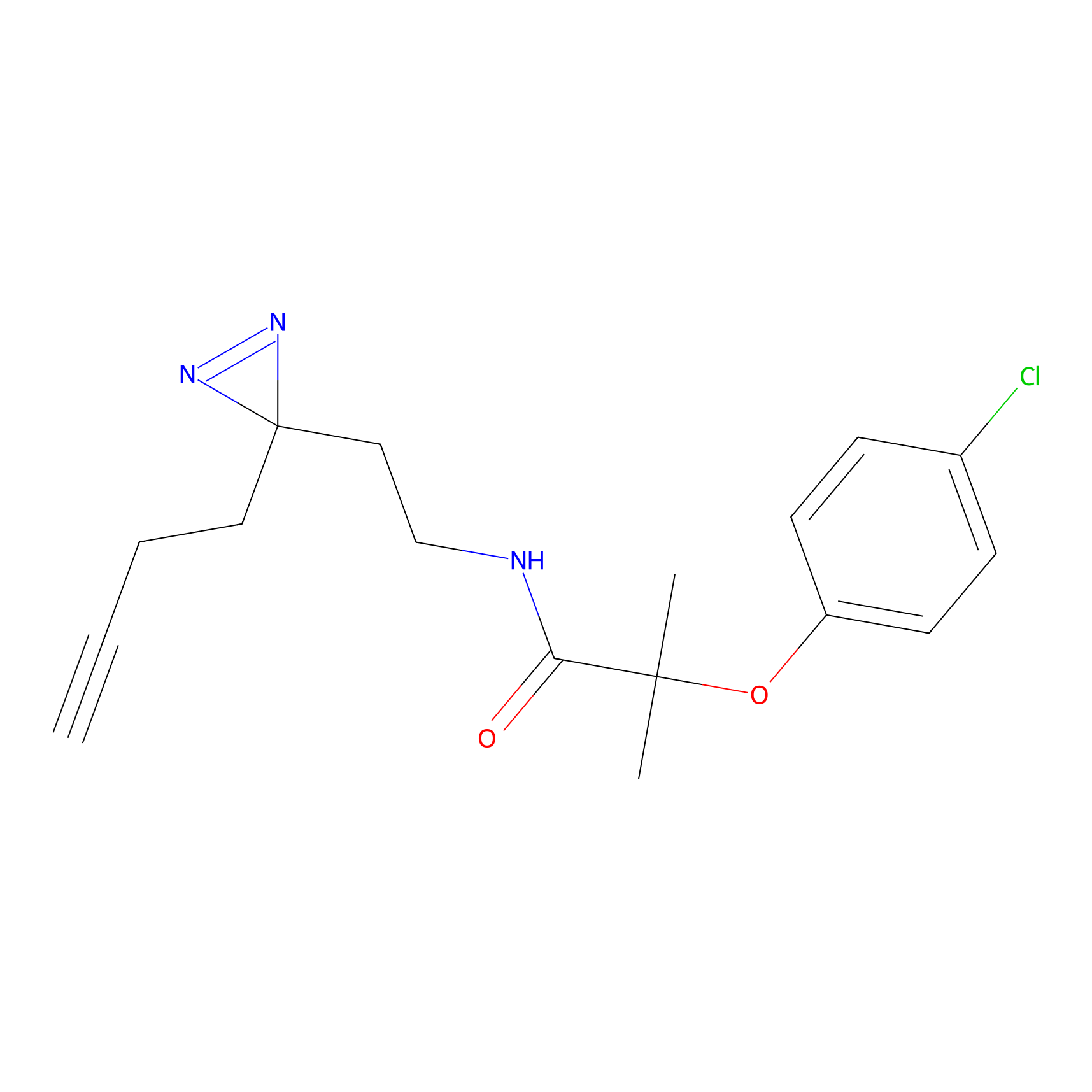
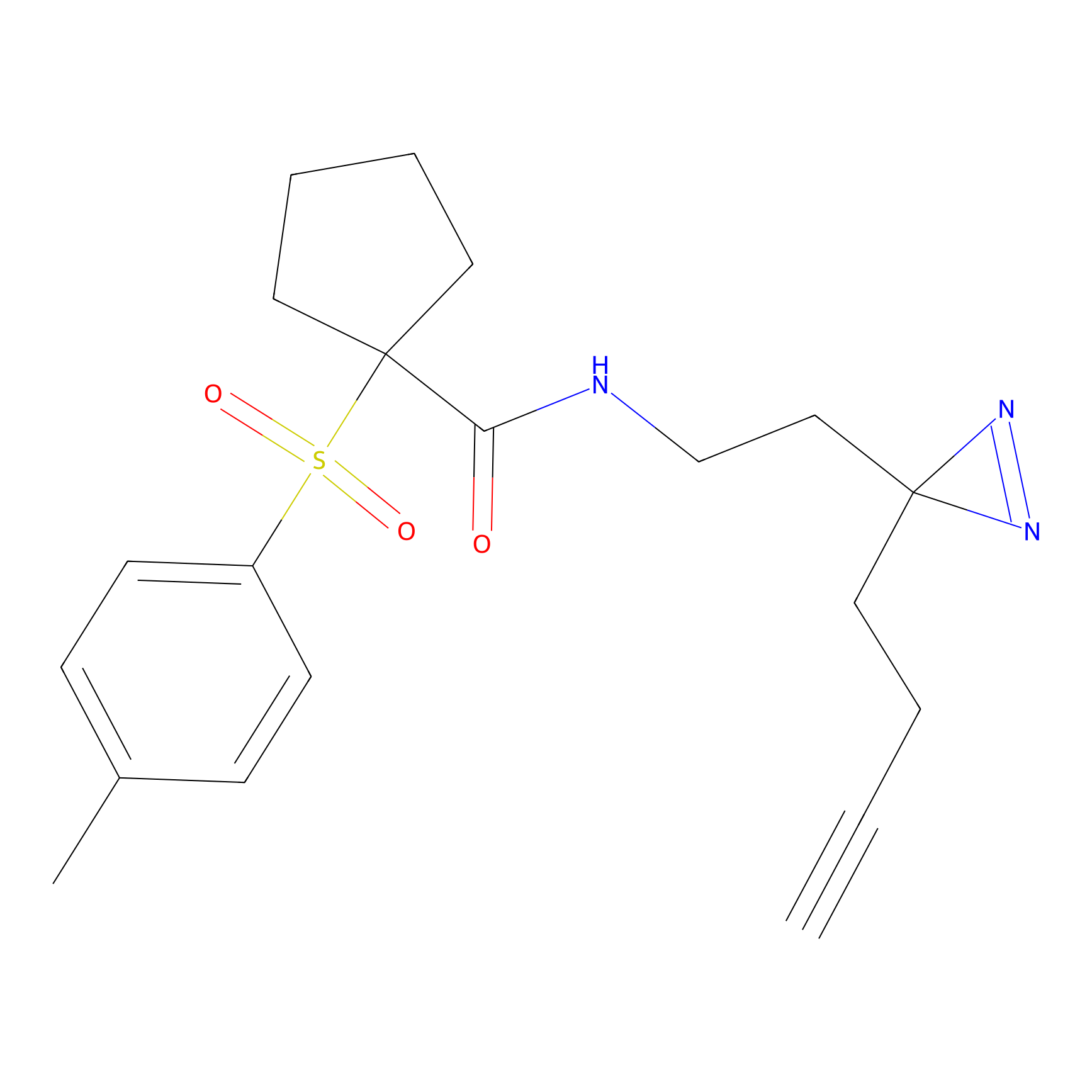
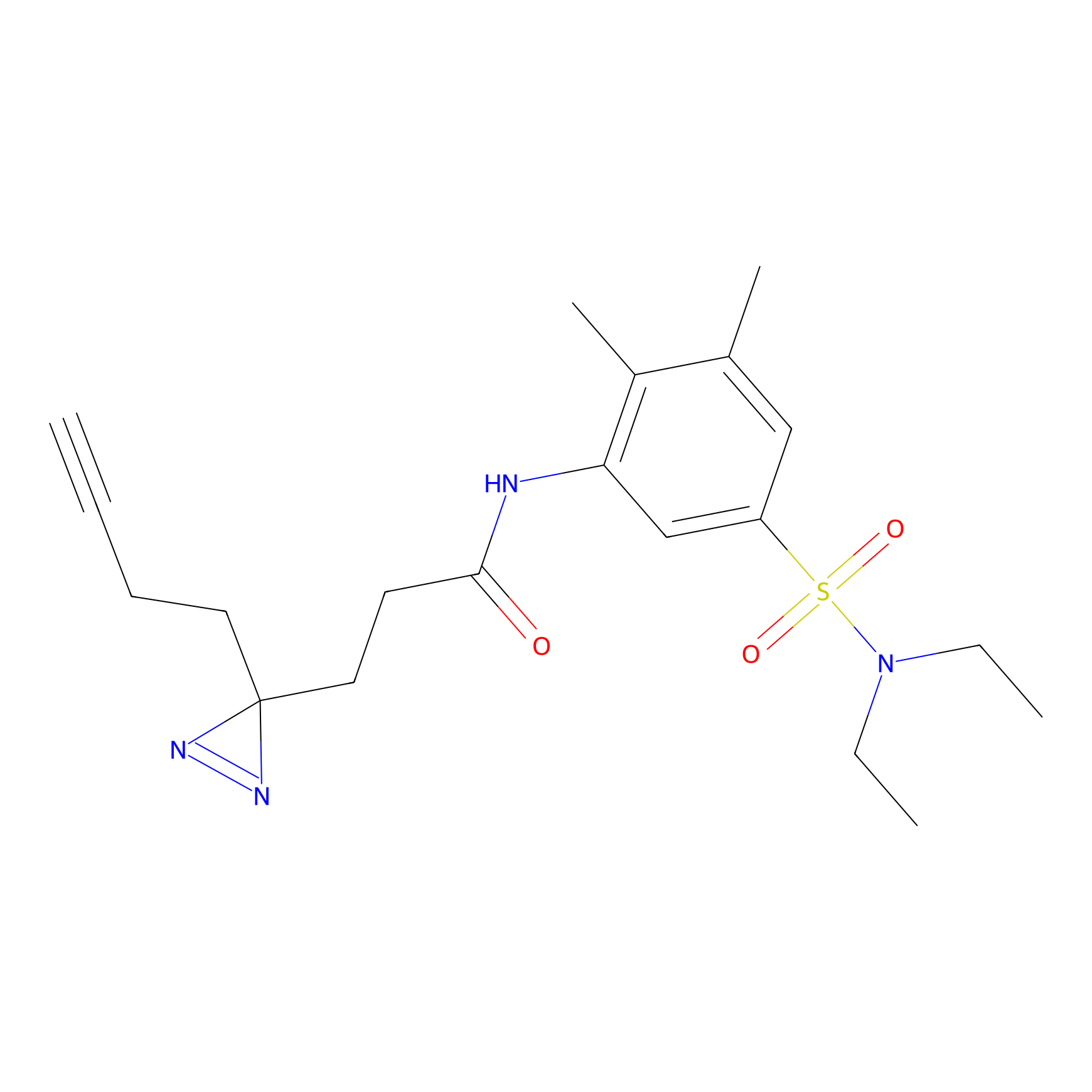
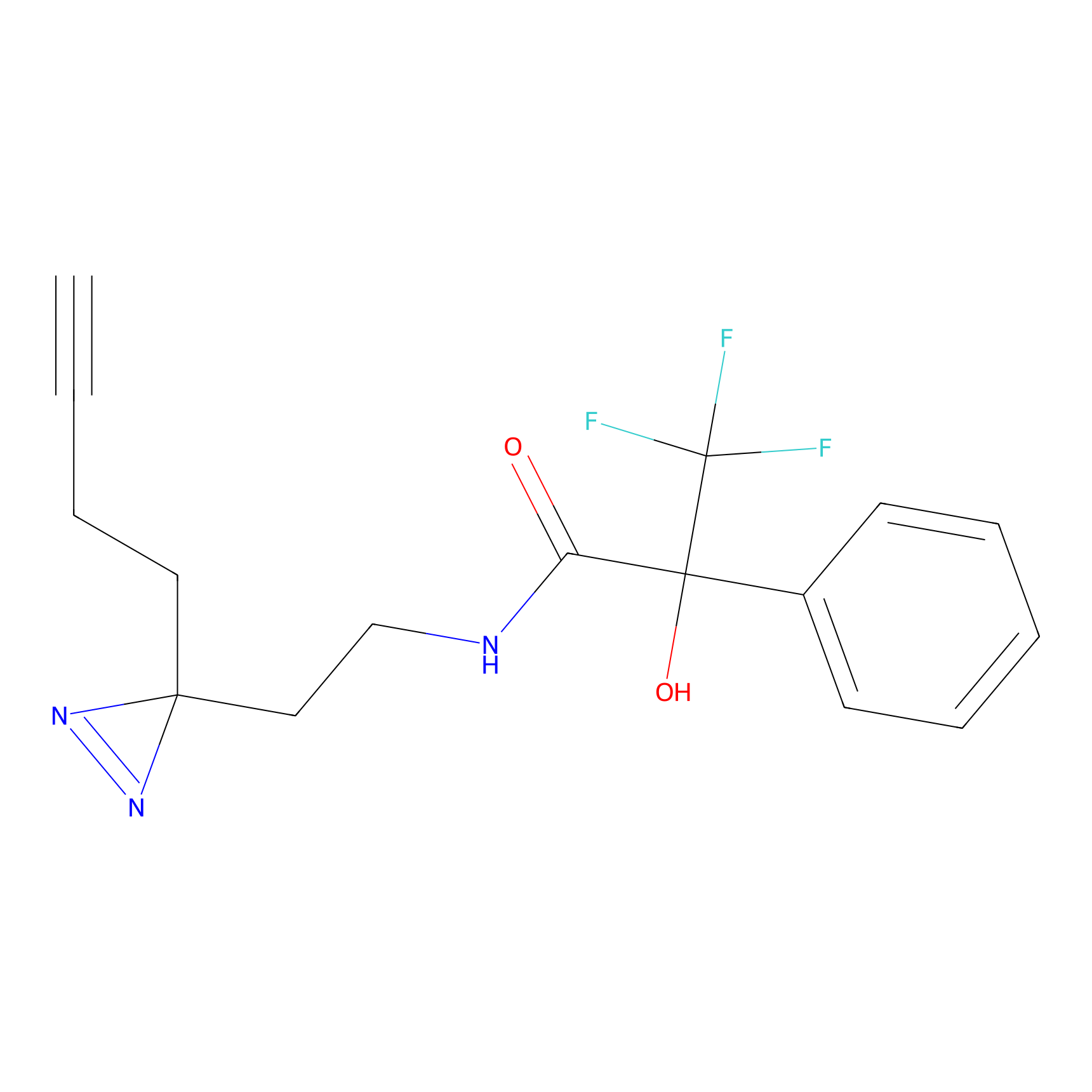
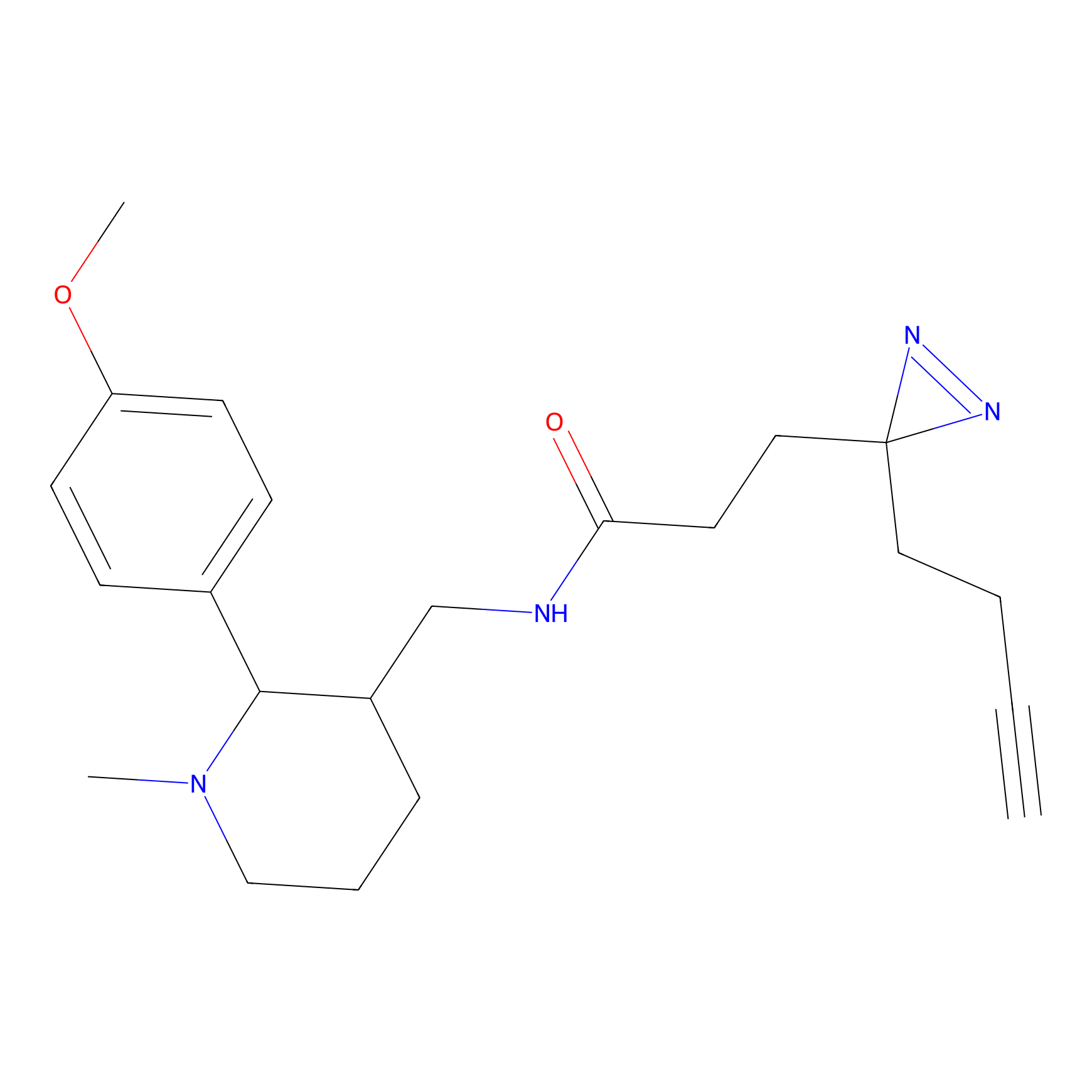
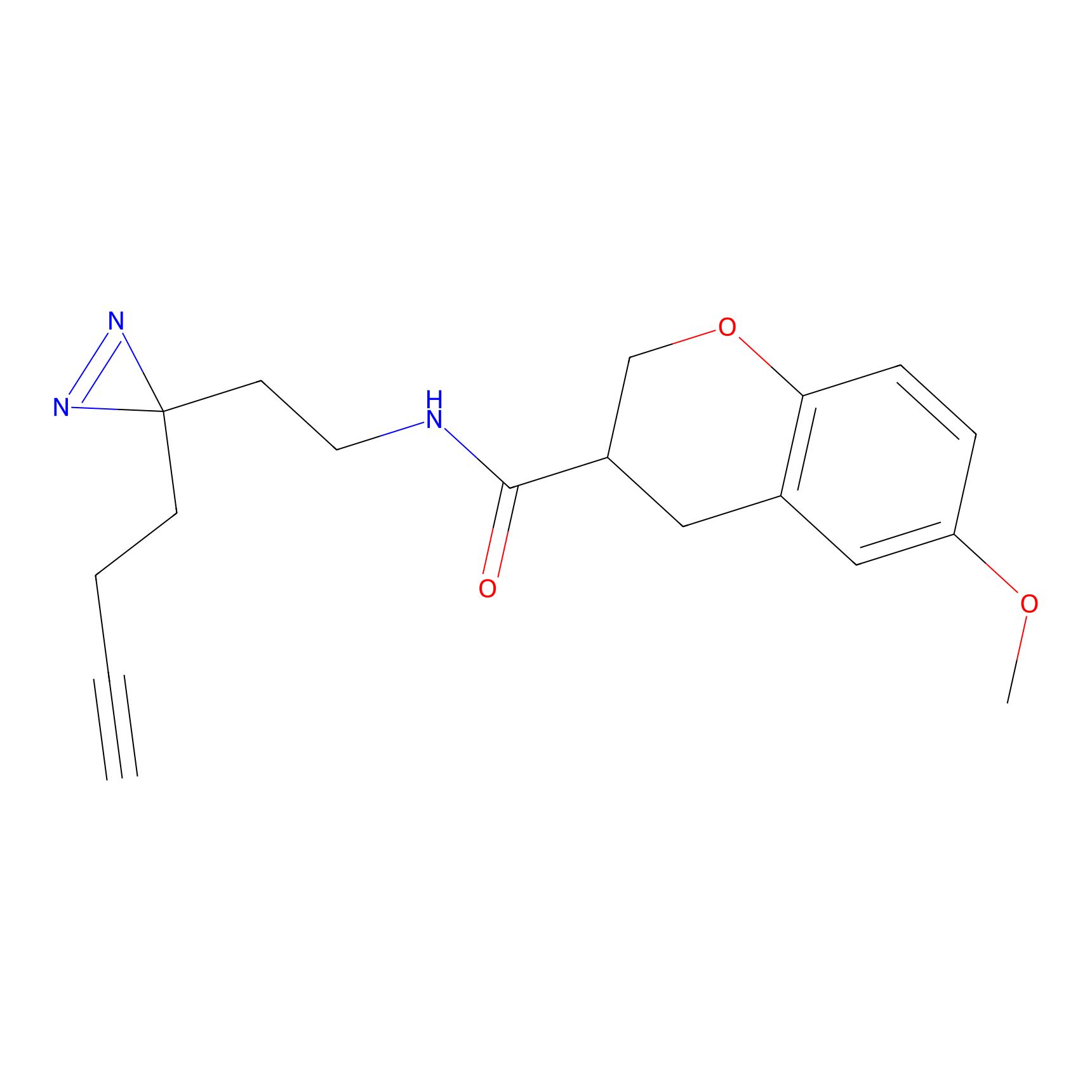
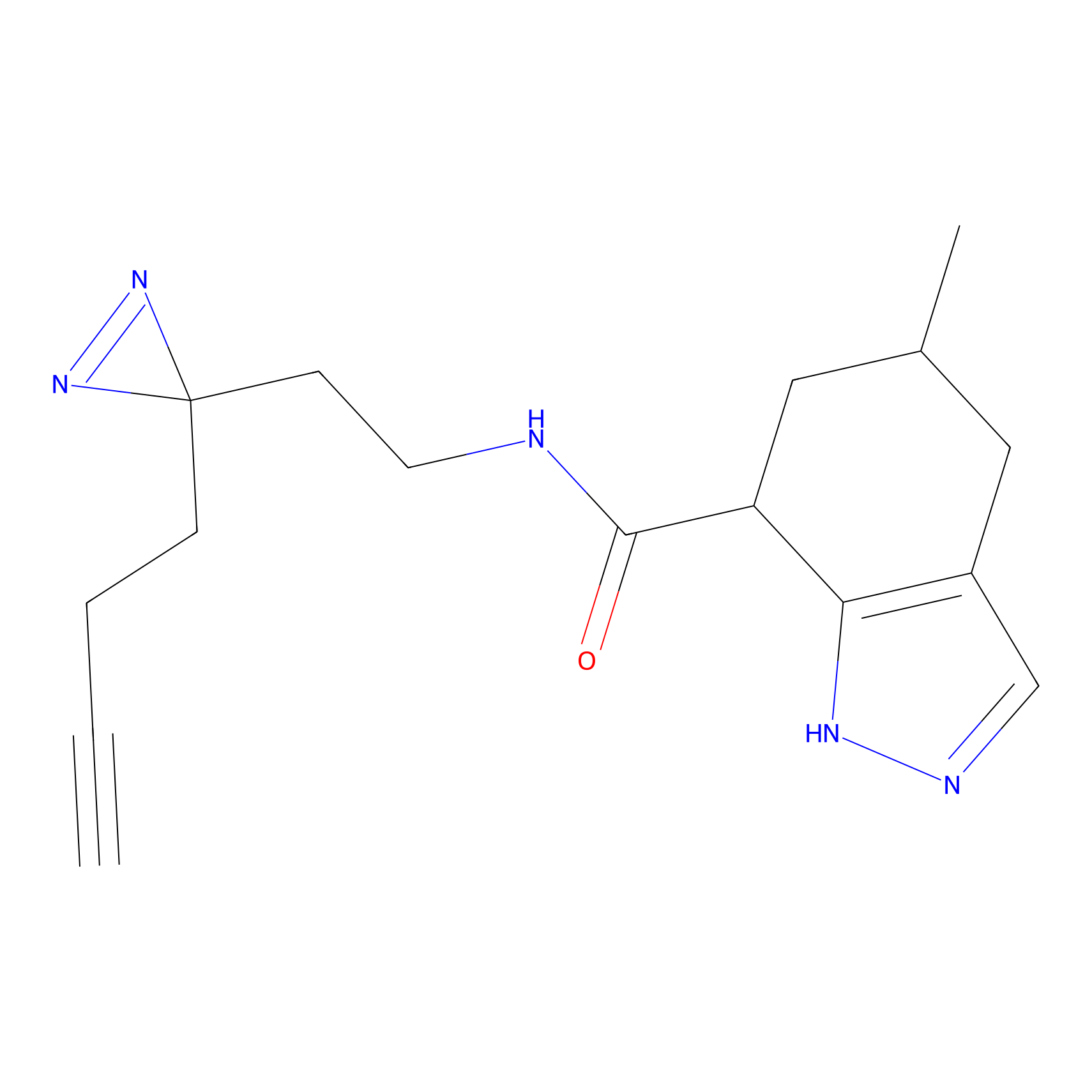
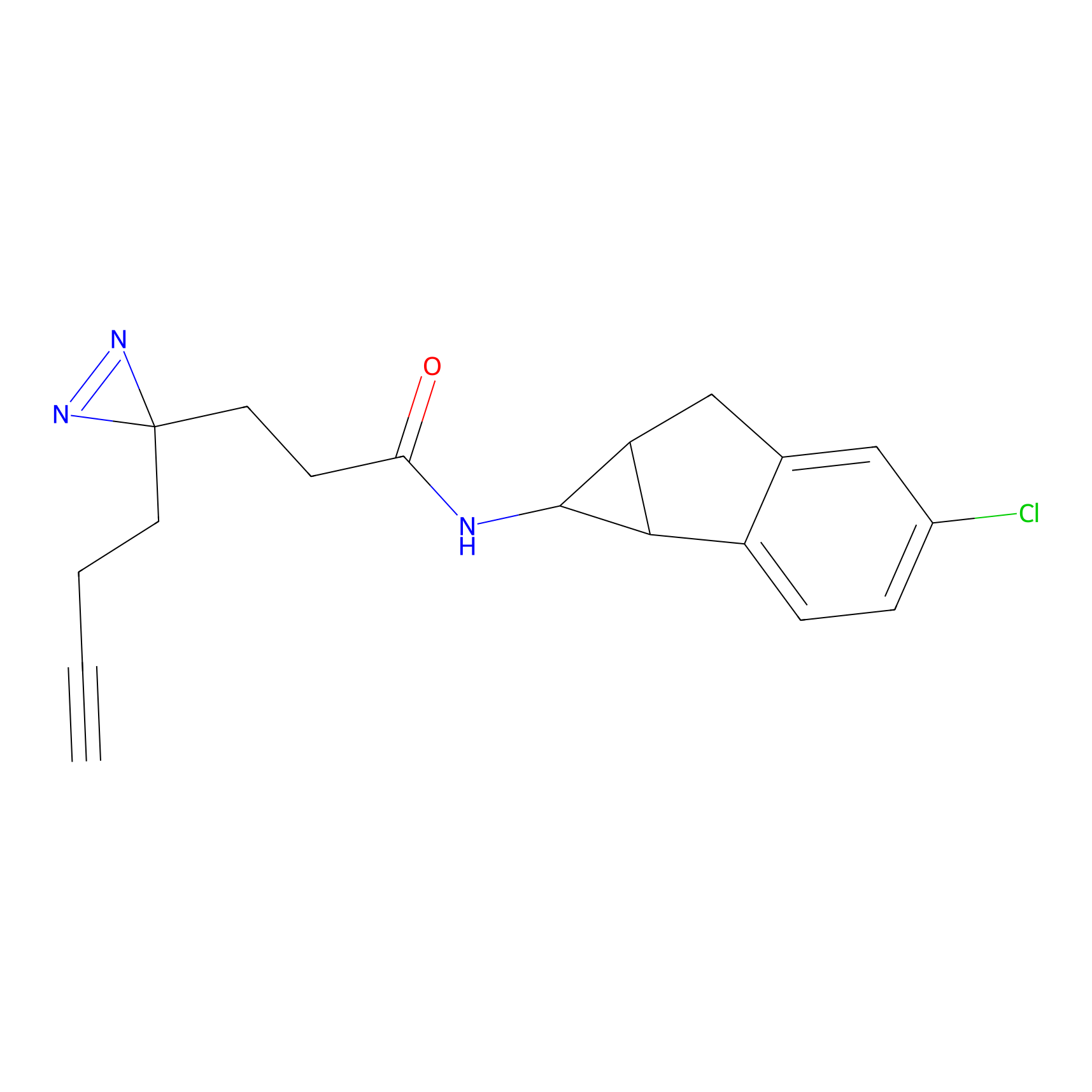
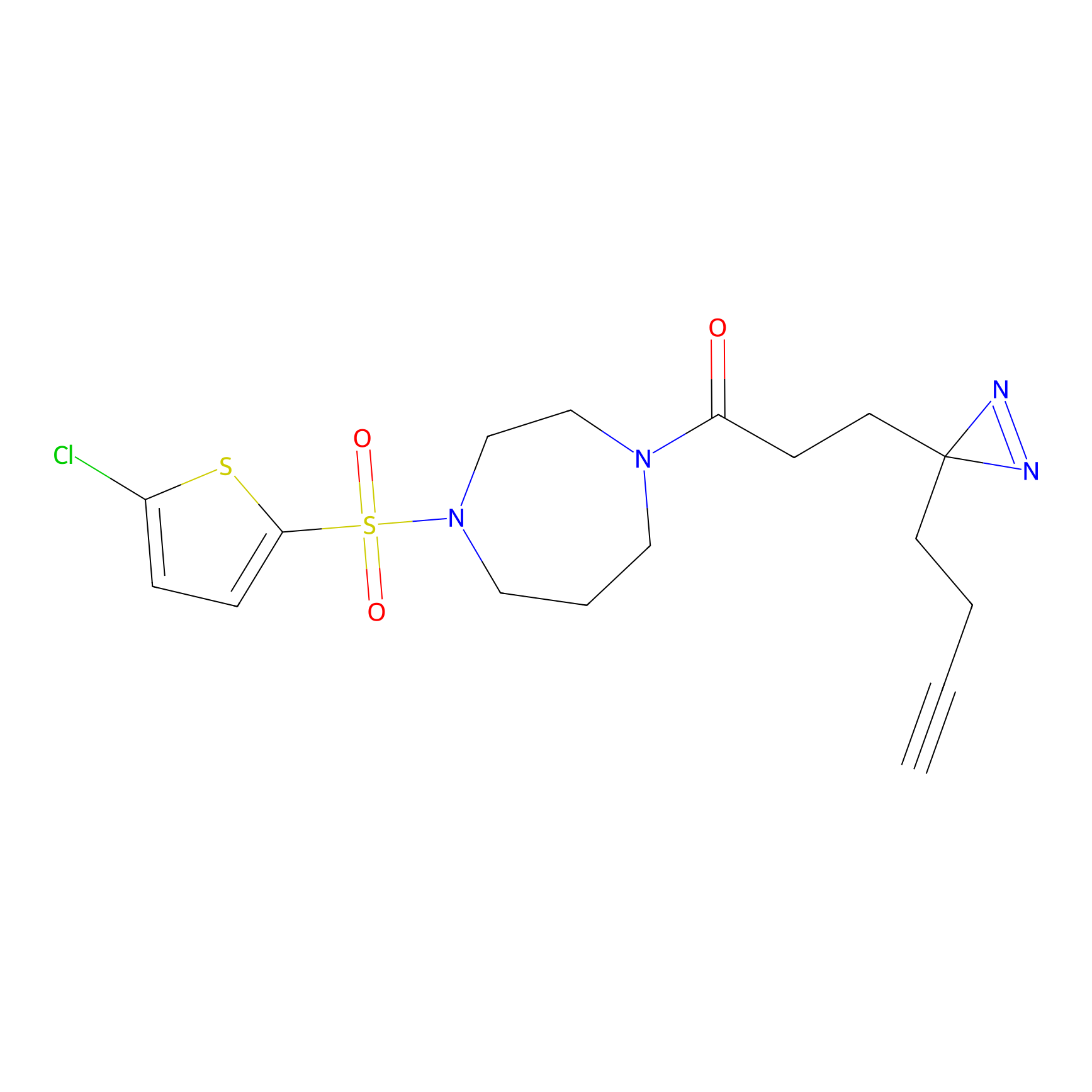
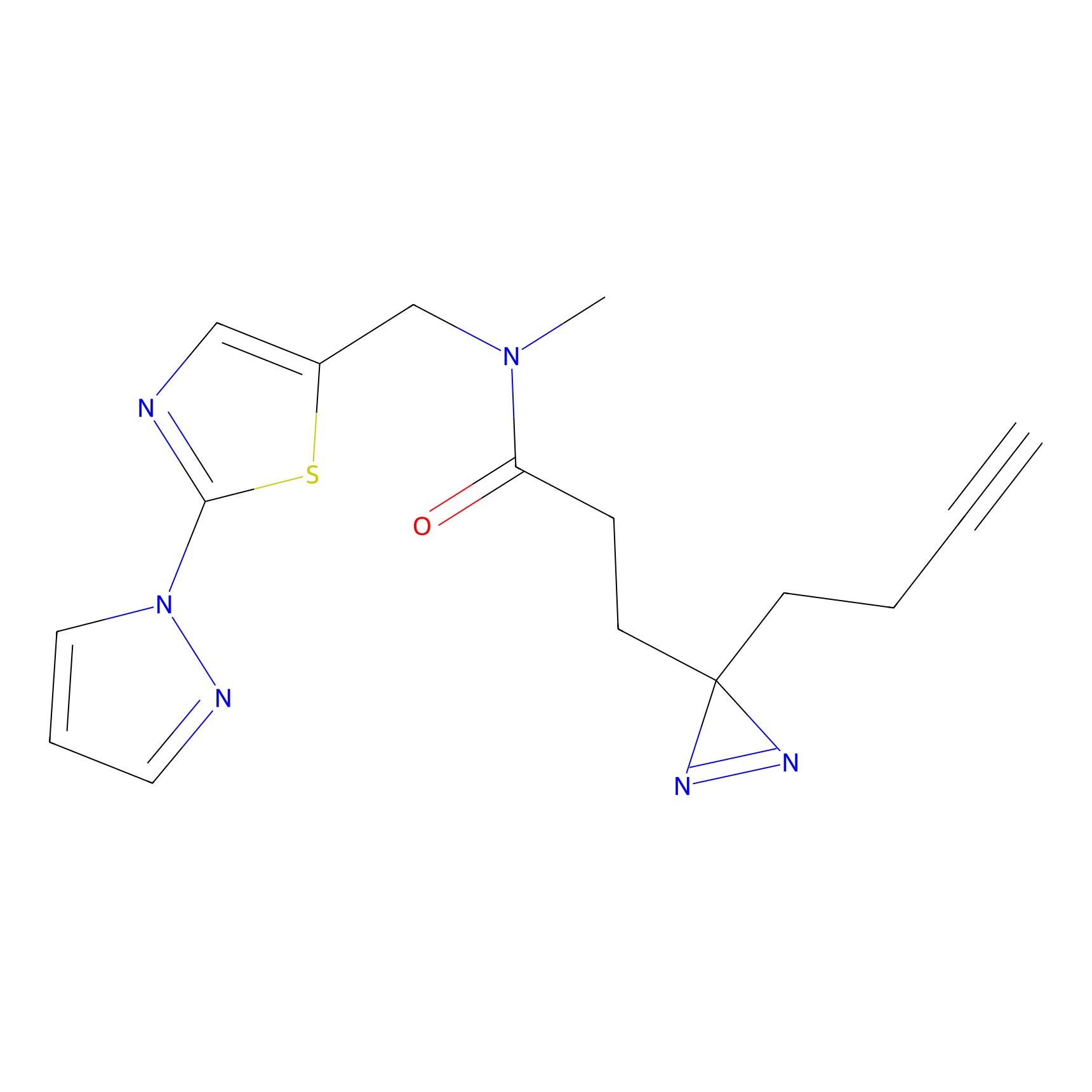
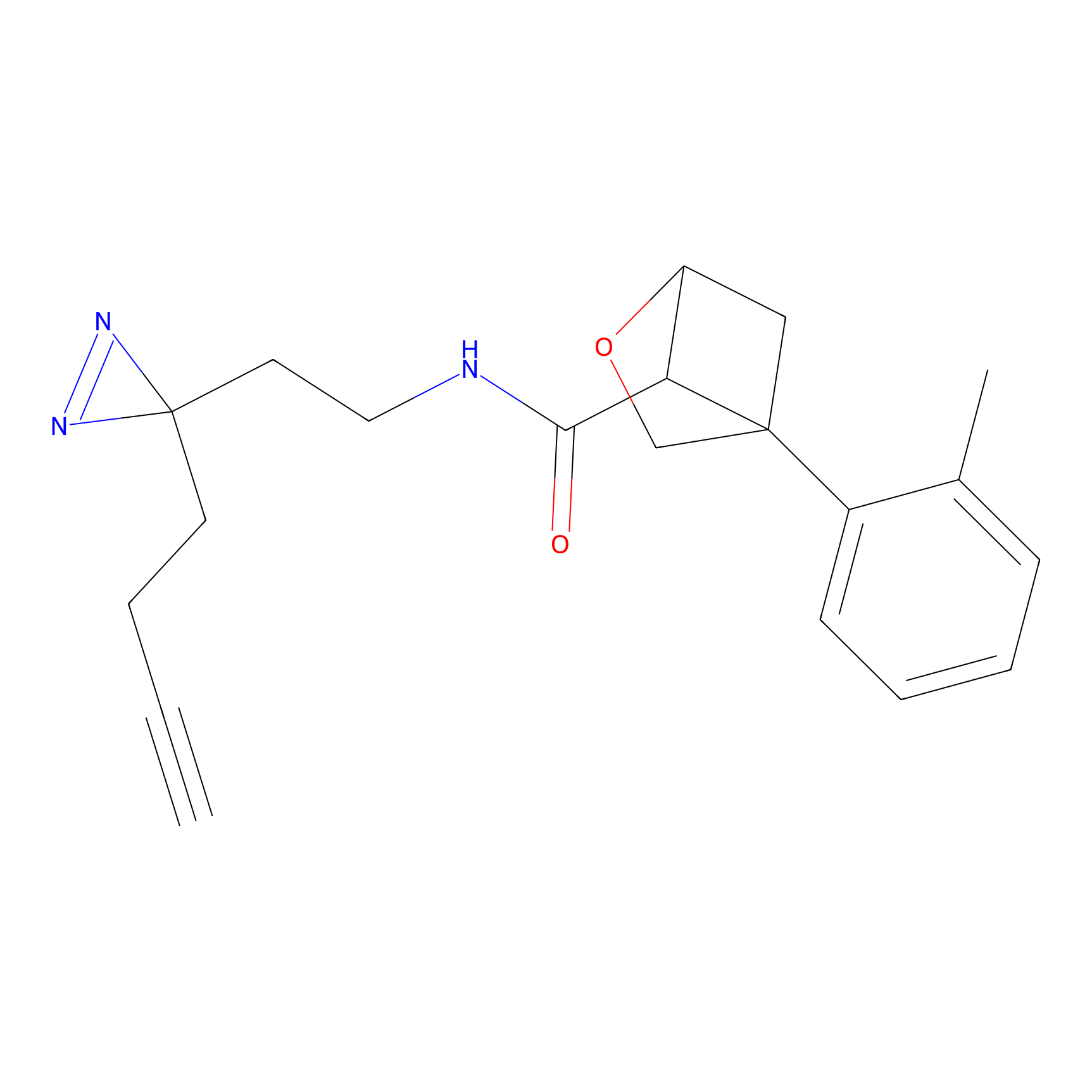
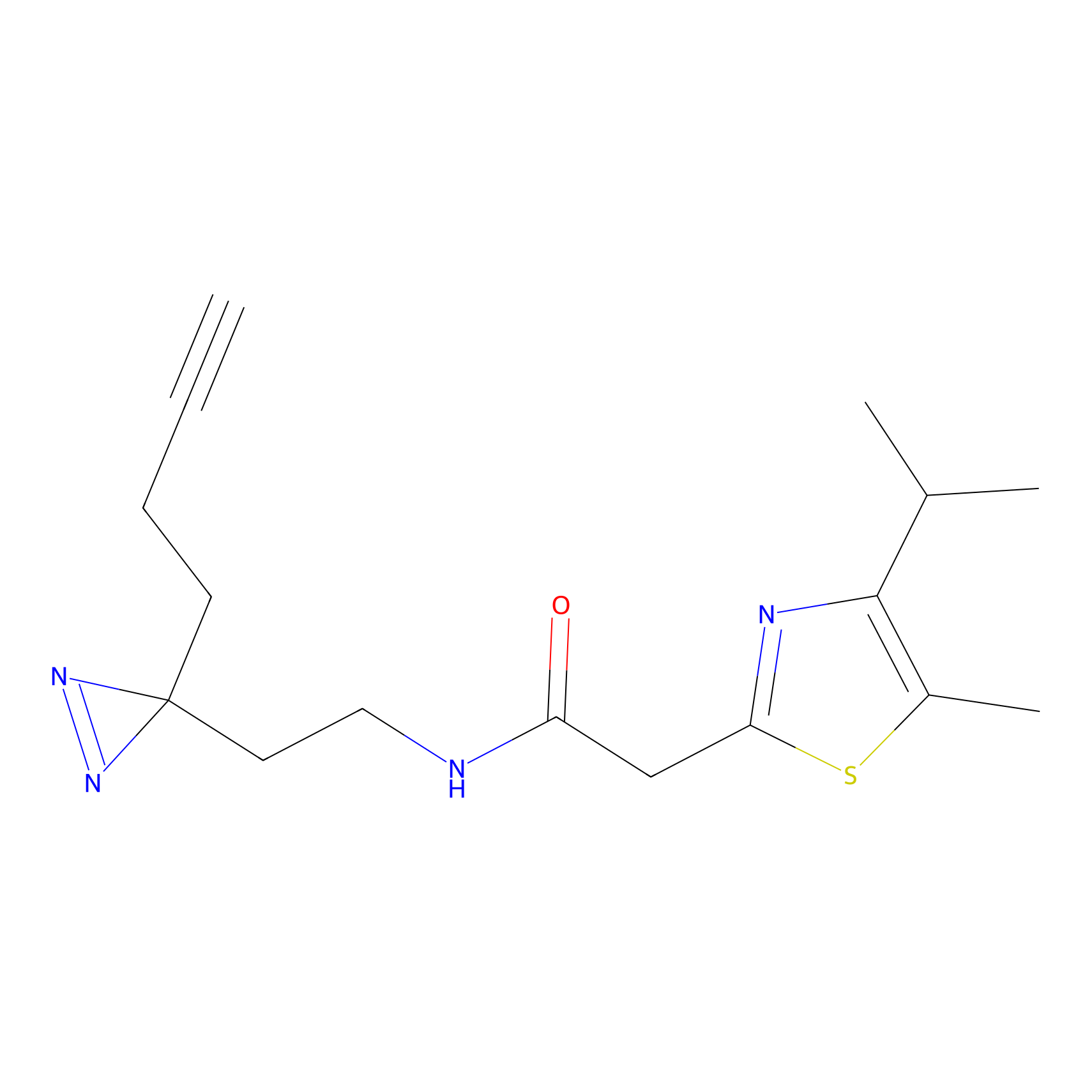
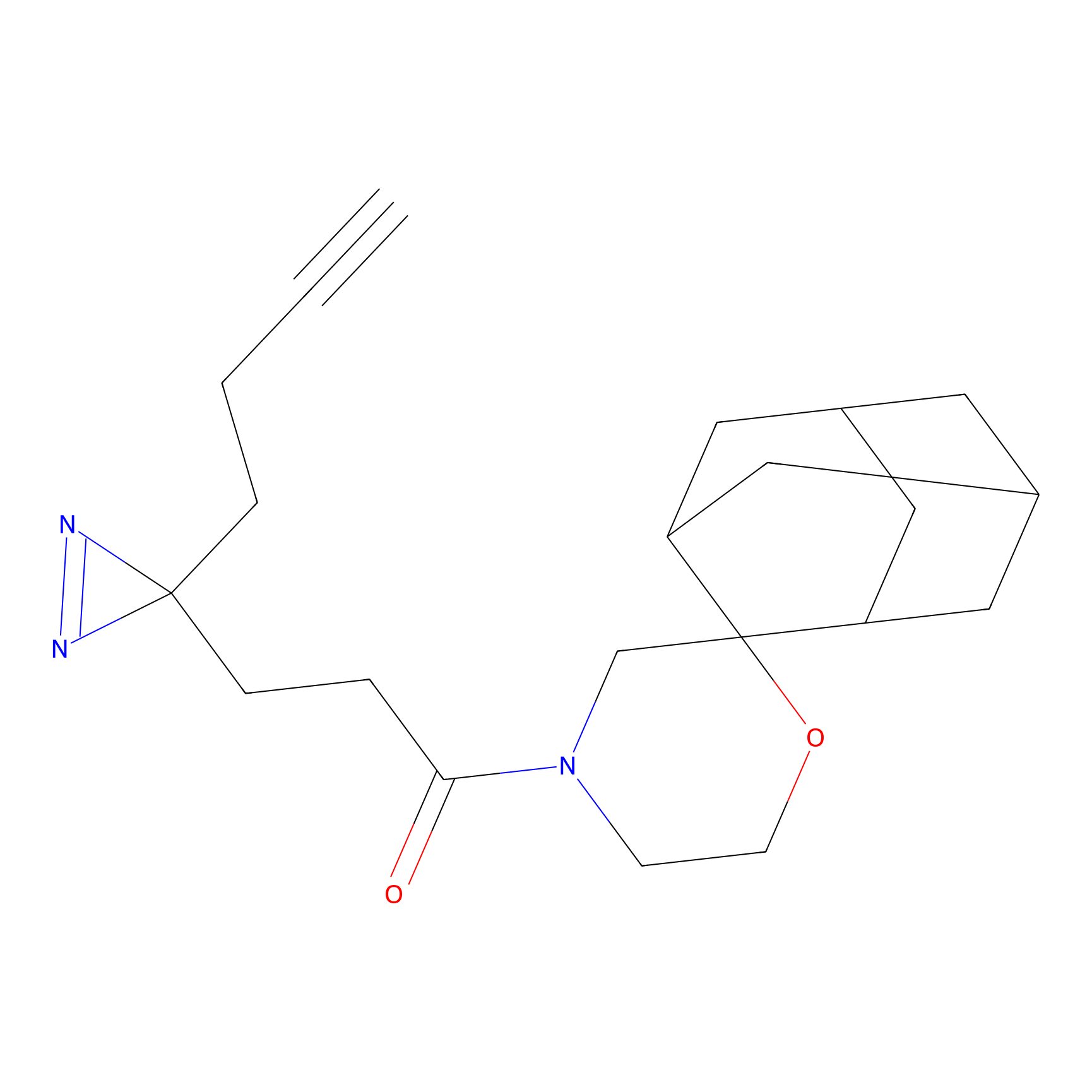
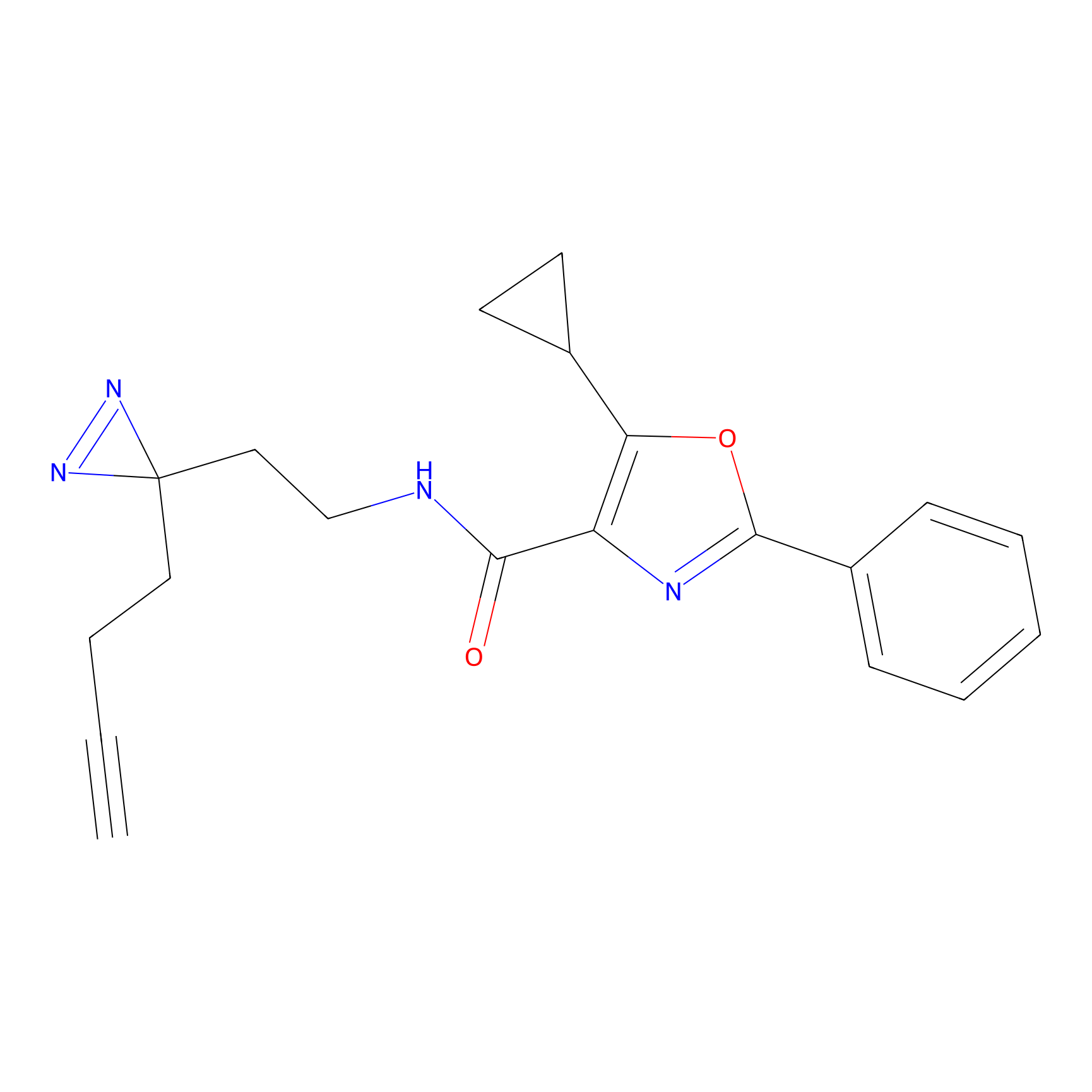
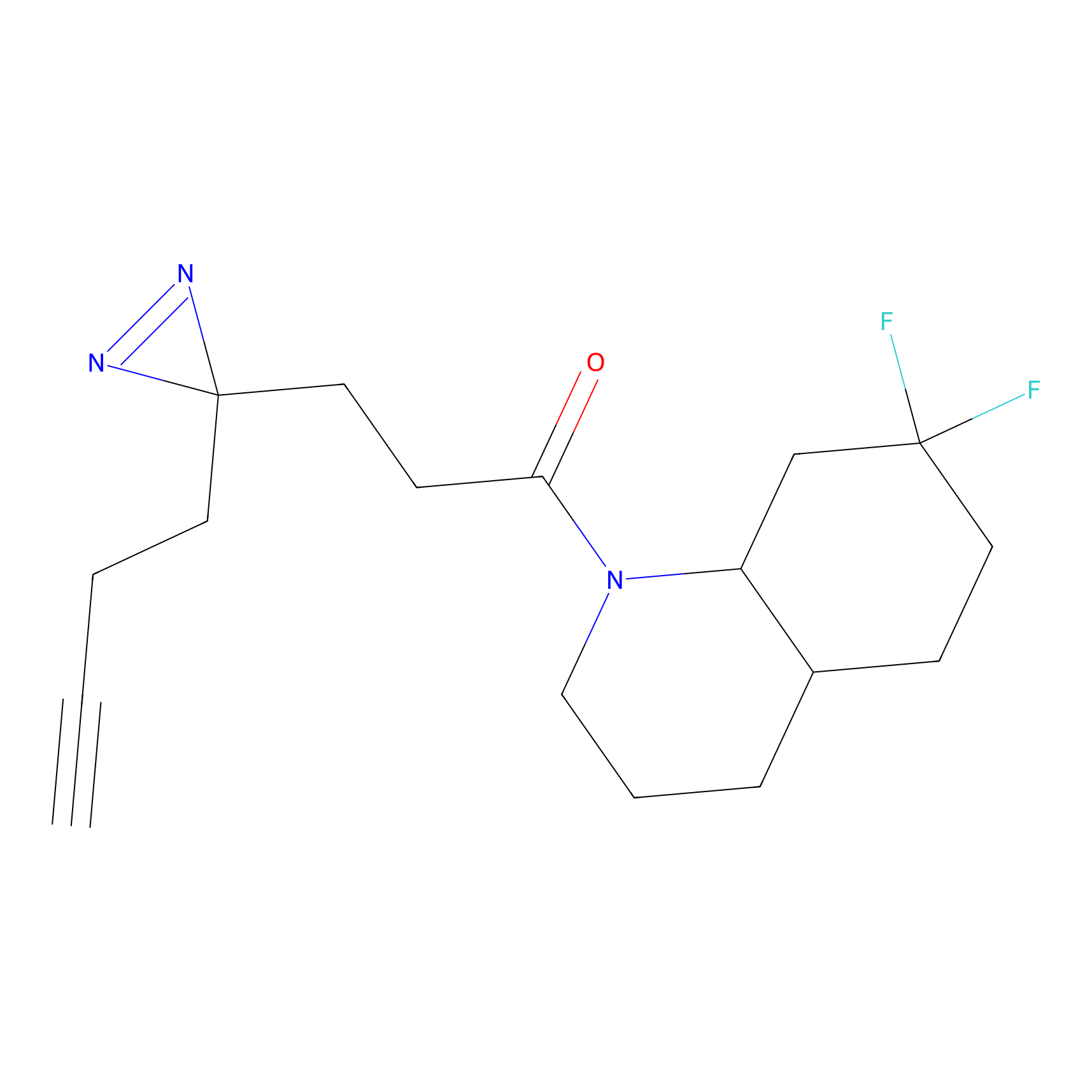
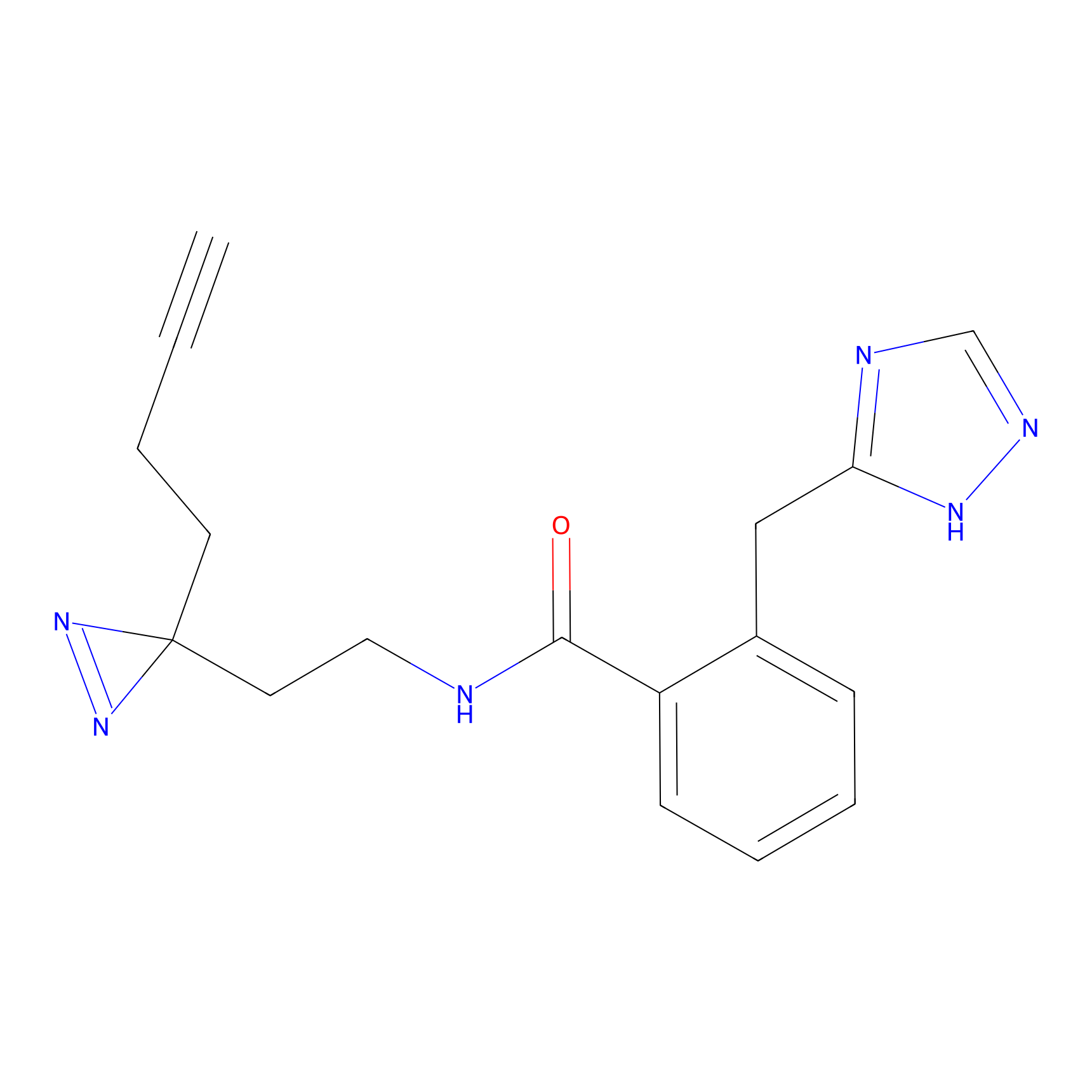
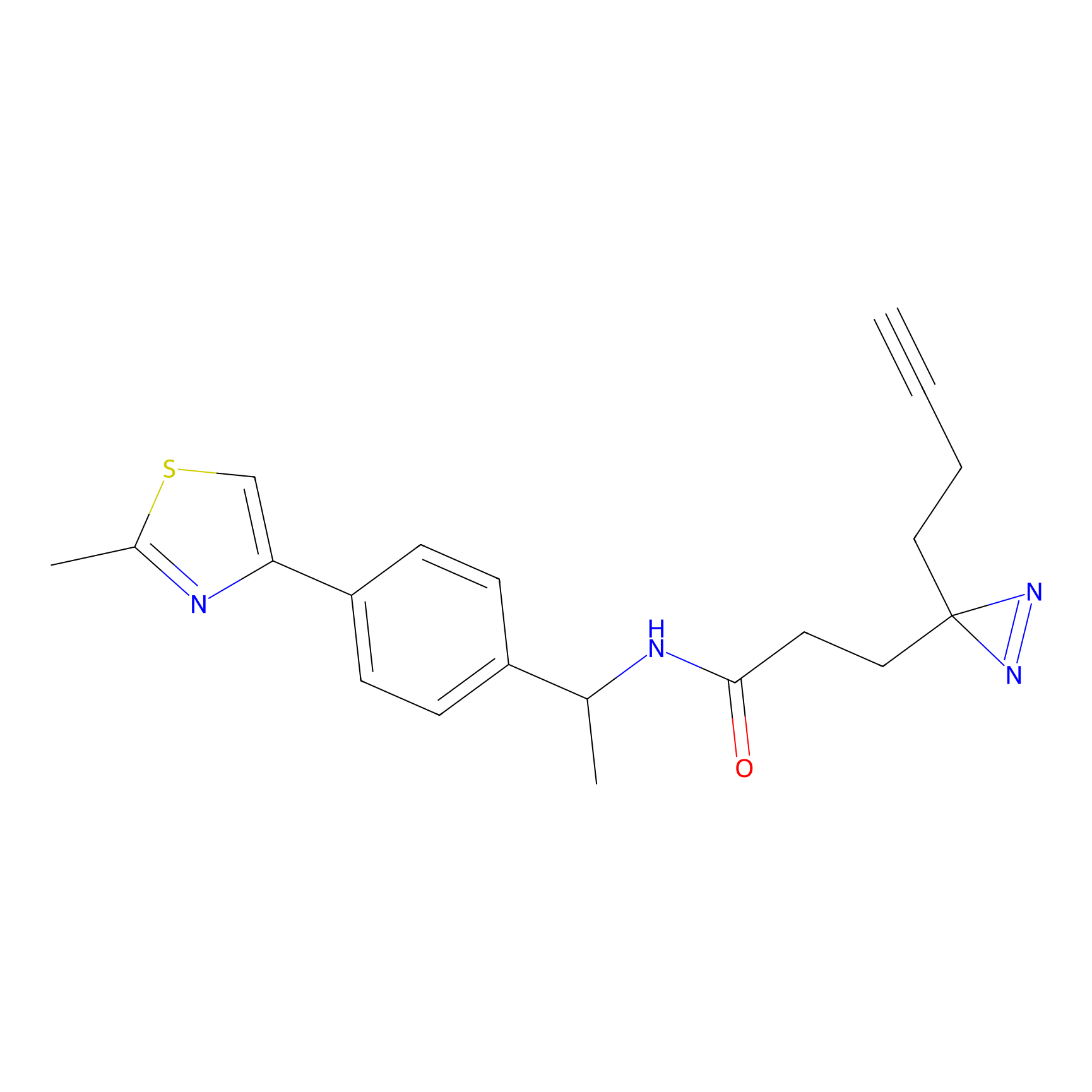
|
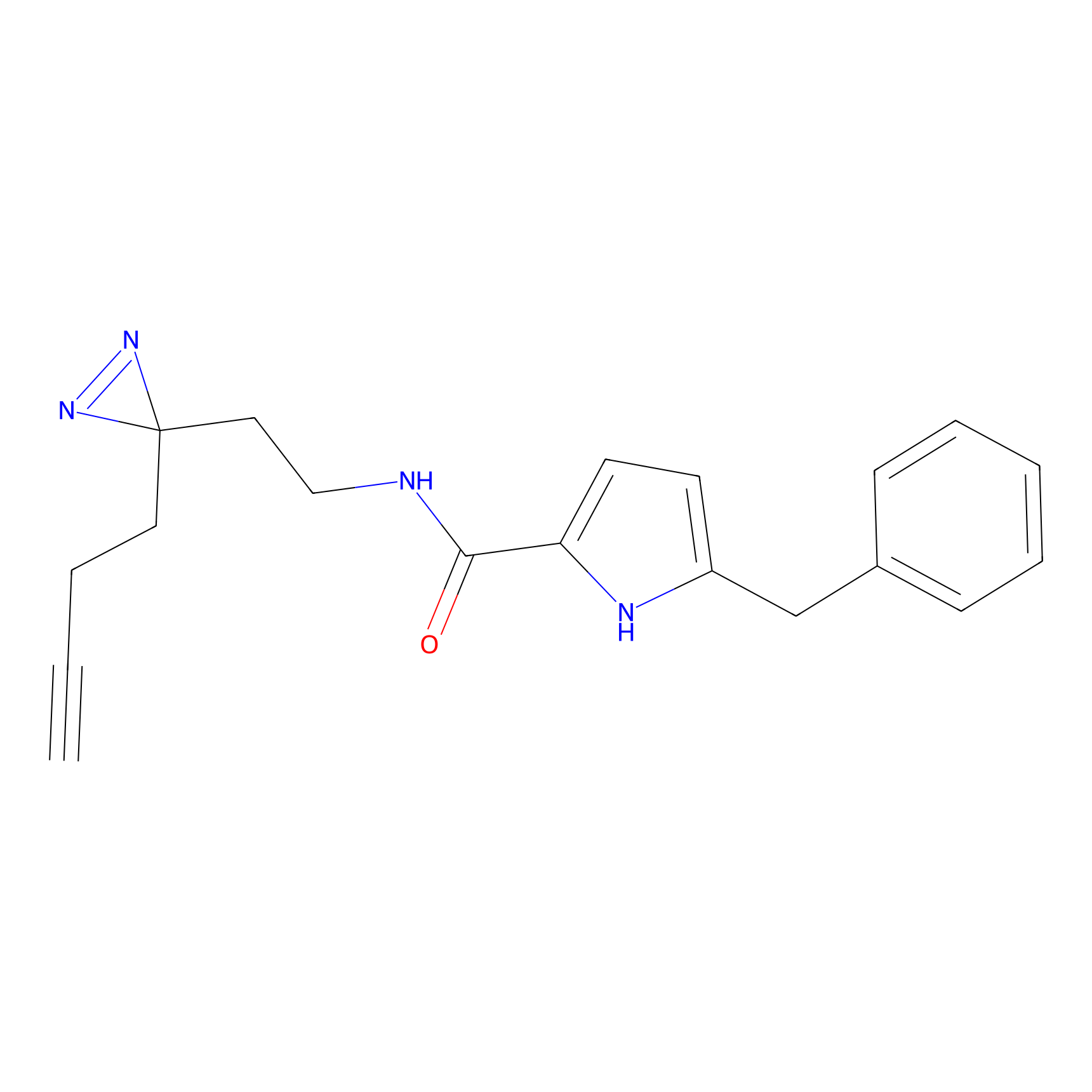
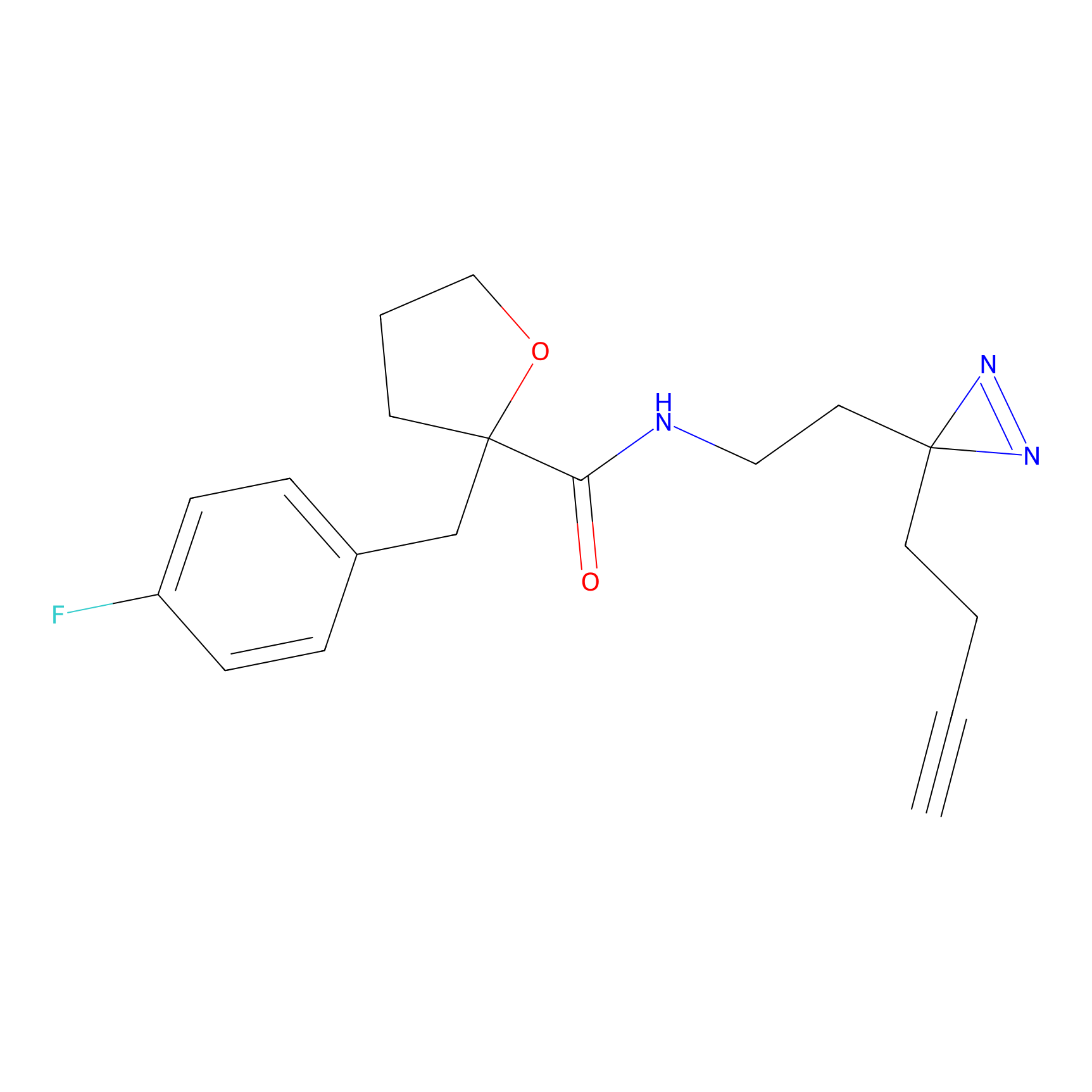
STPyne Probe Info |
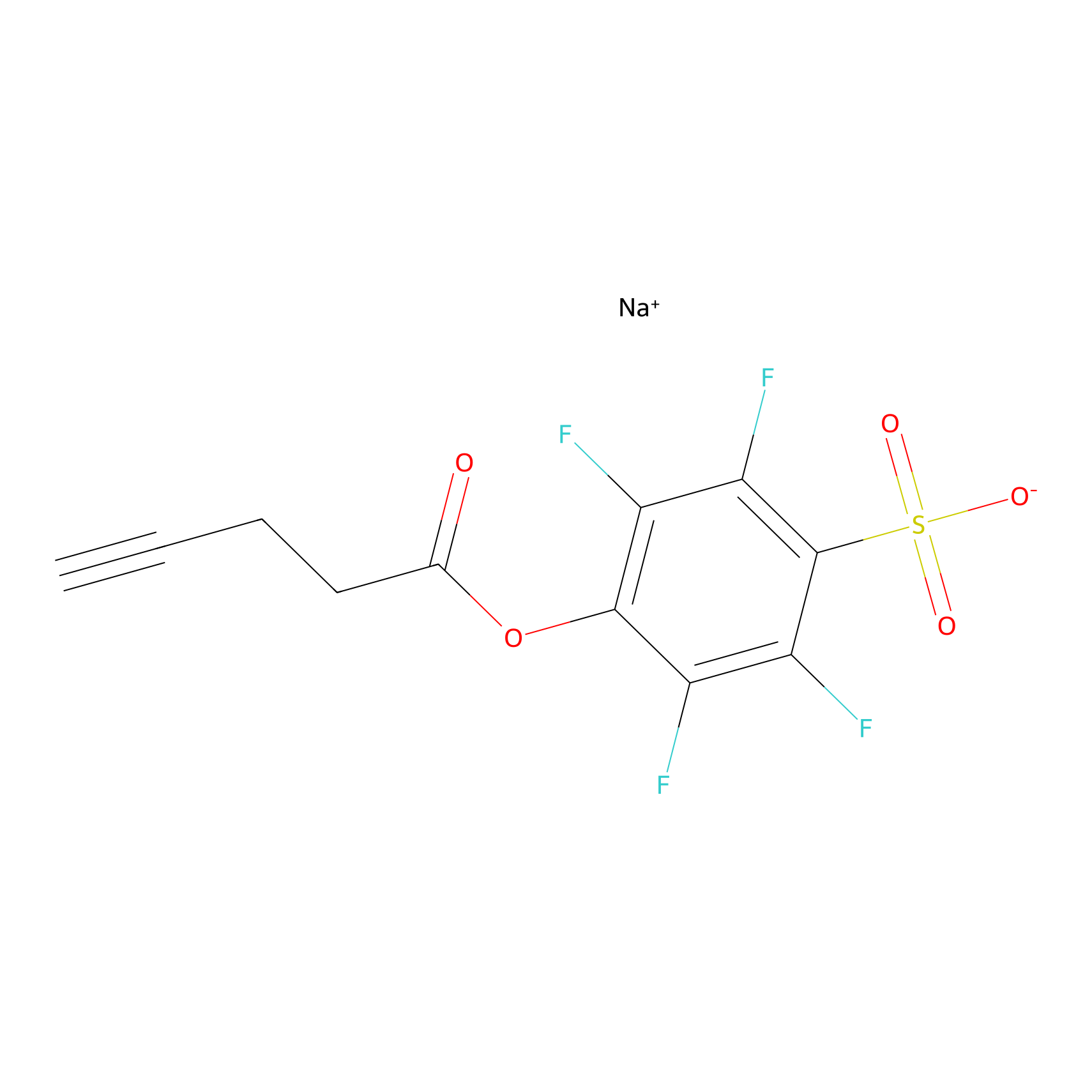 |
K239(7.14) | LDD0277 | [2] | |
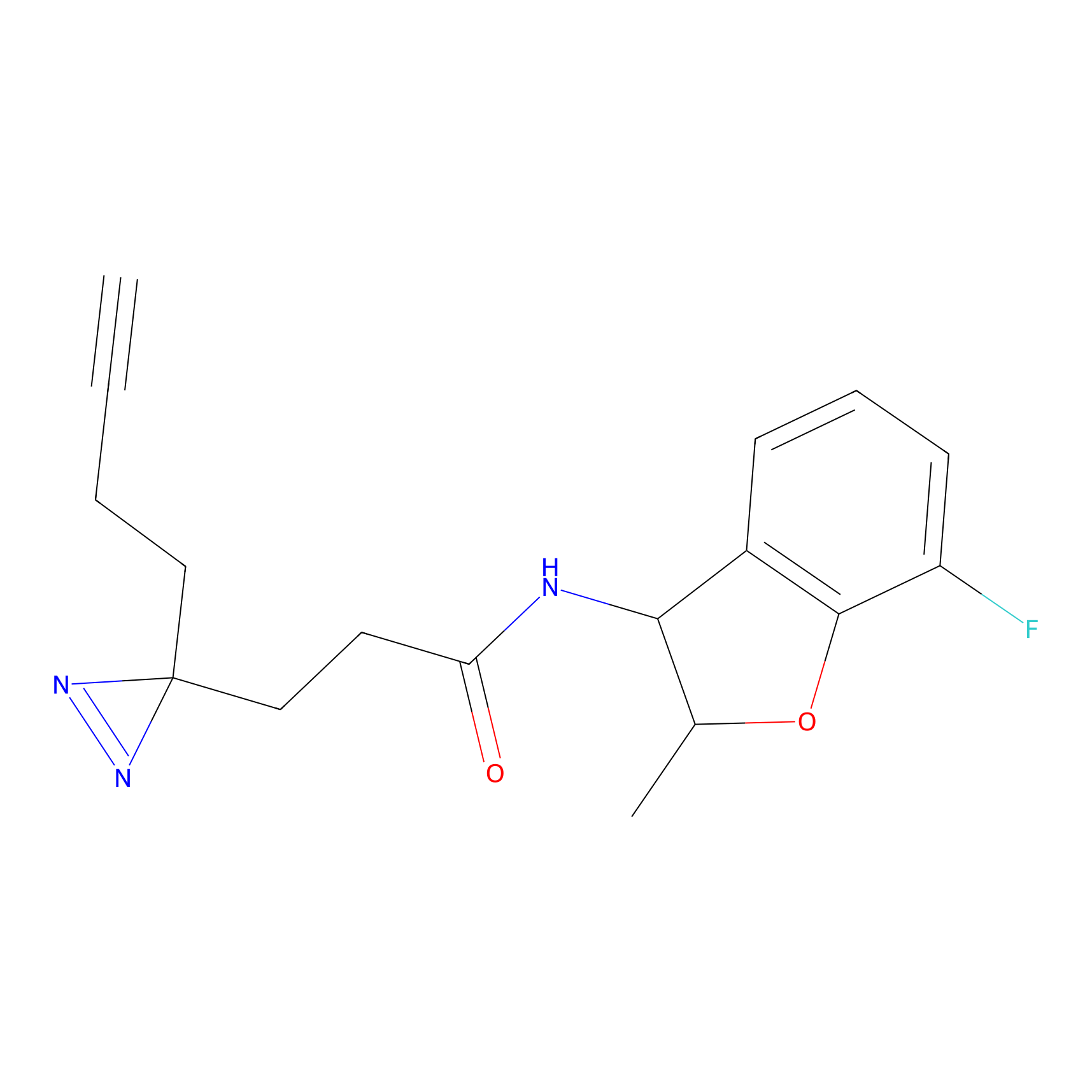
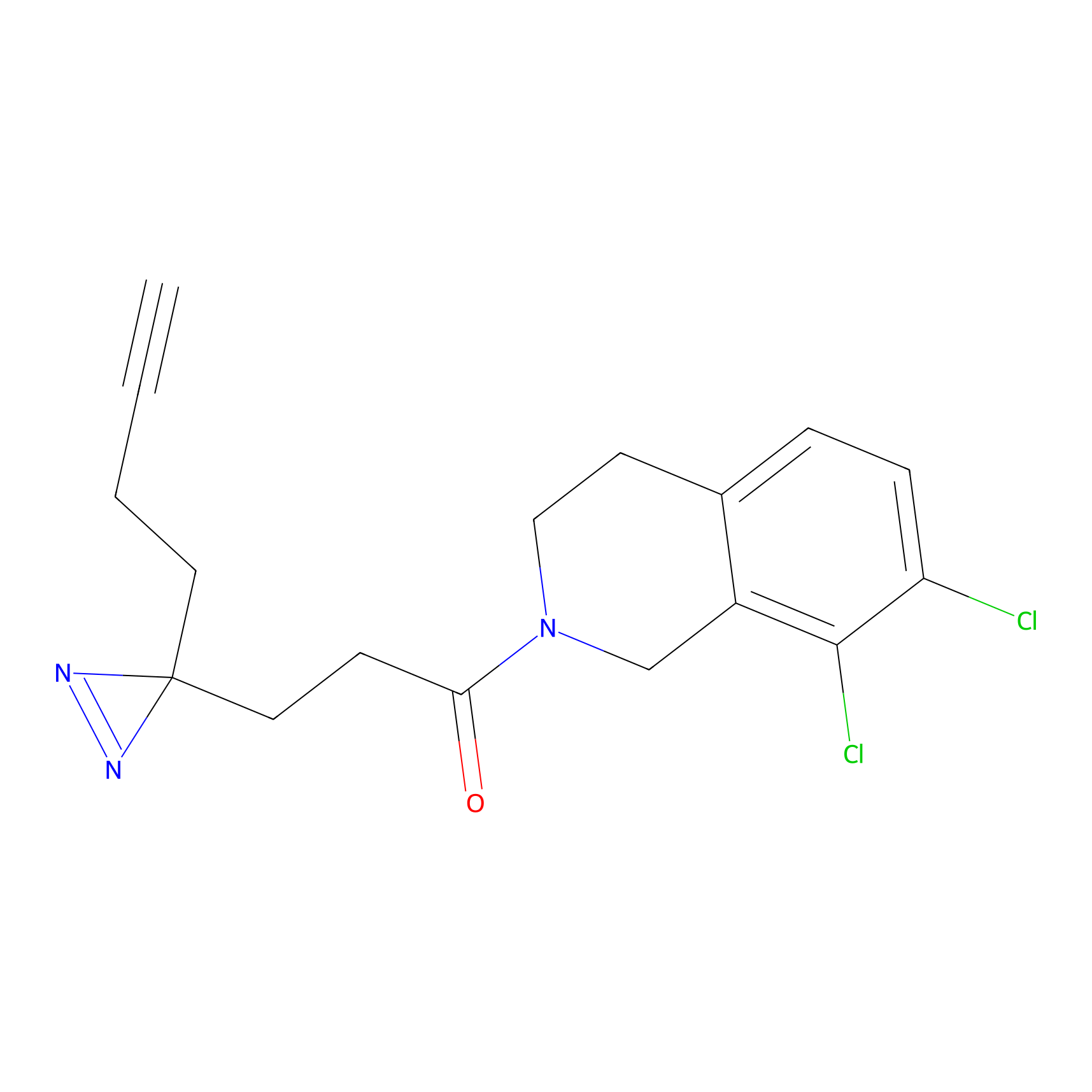
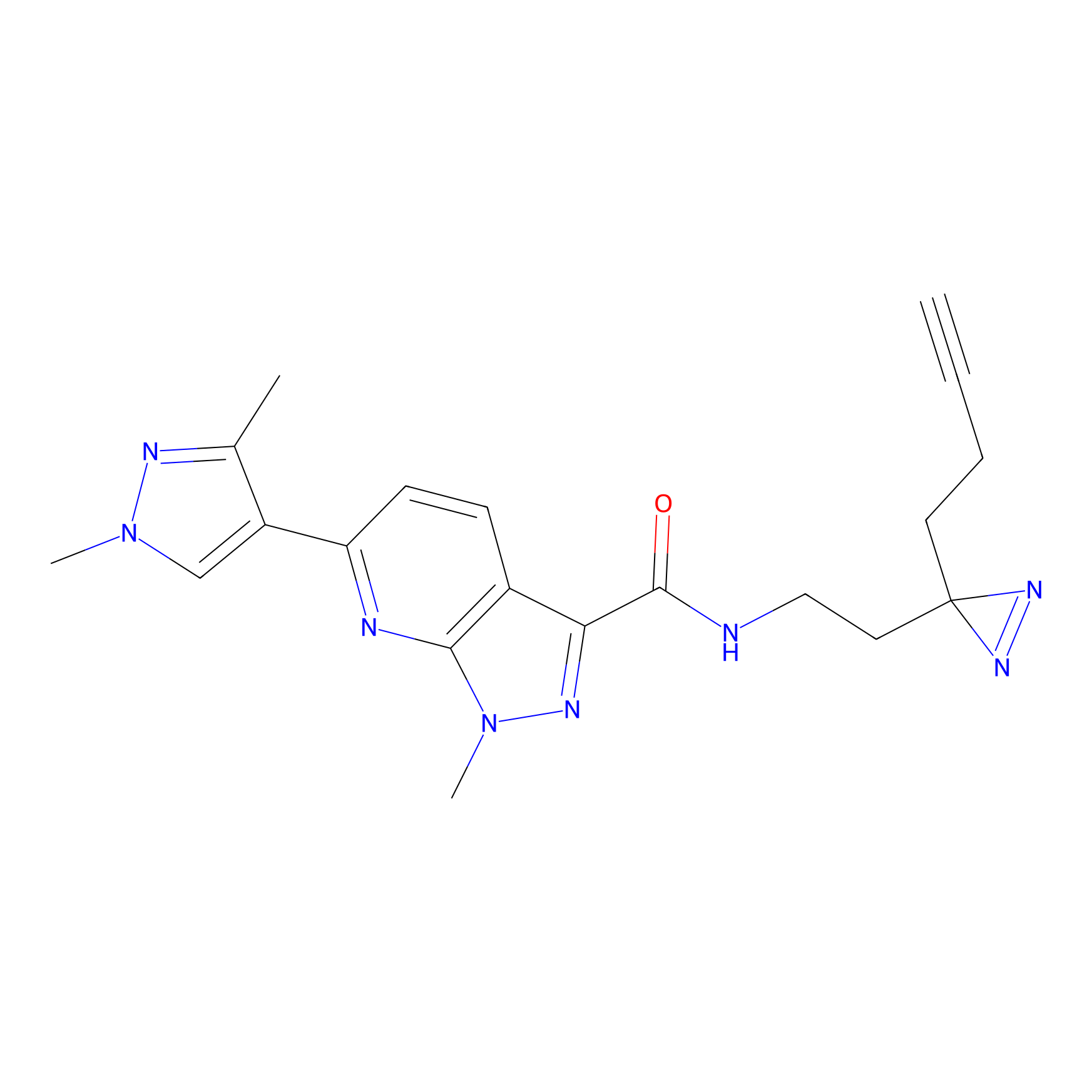
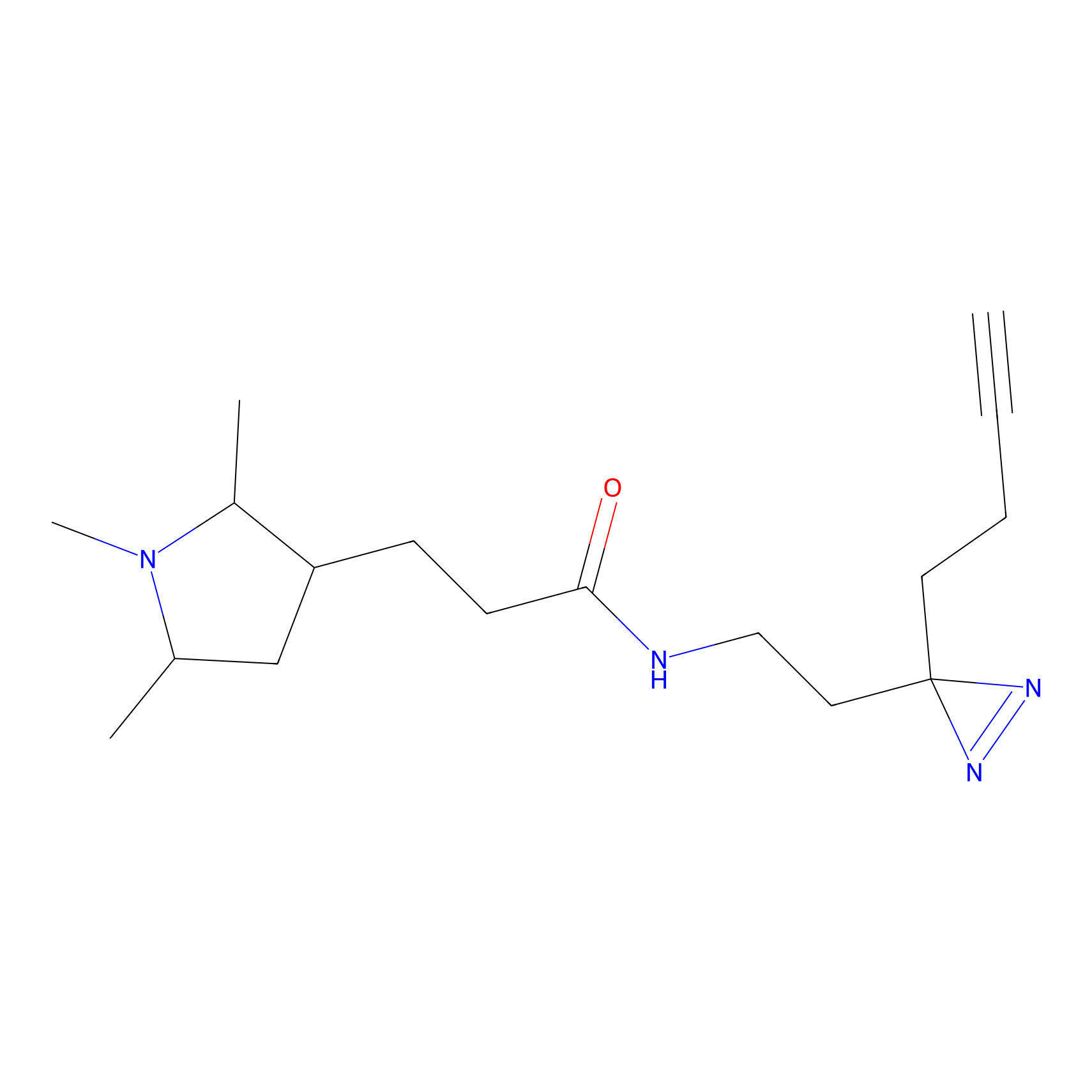
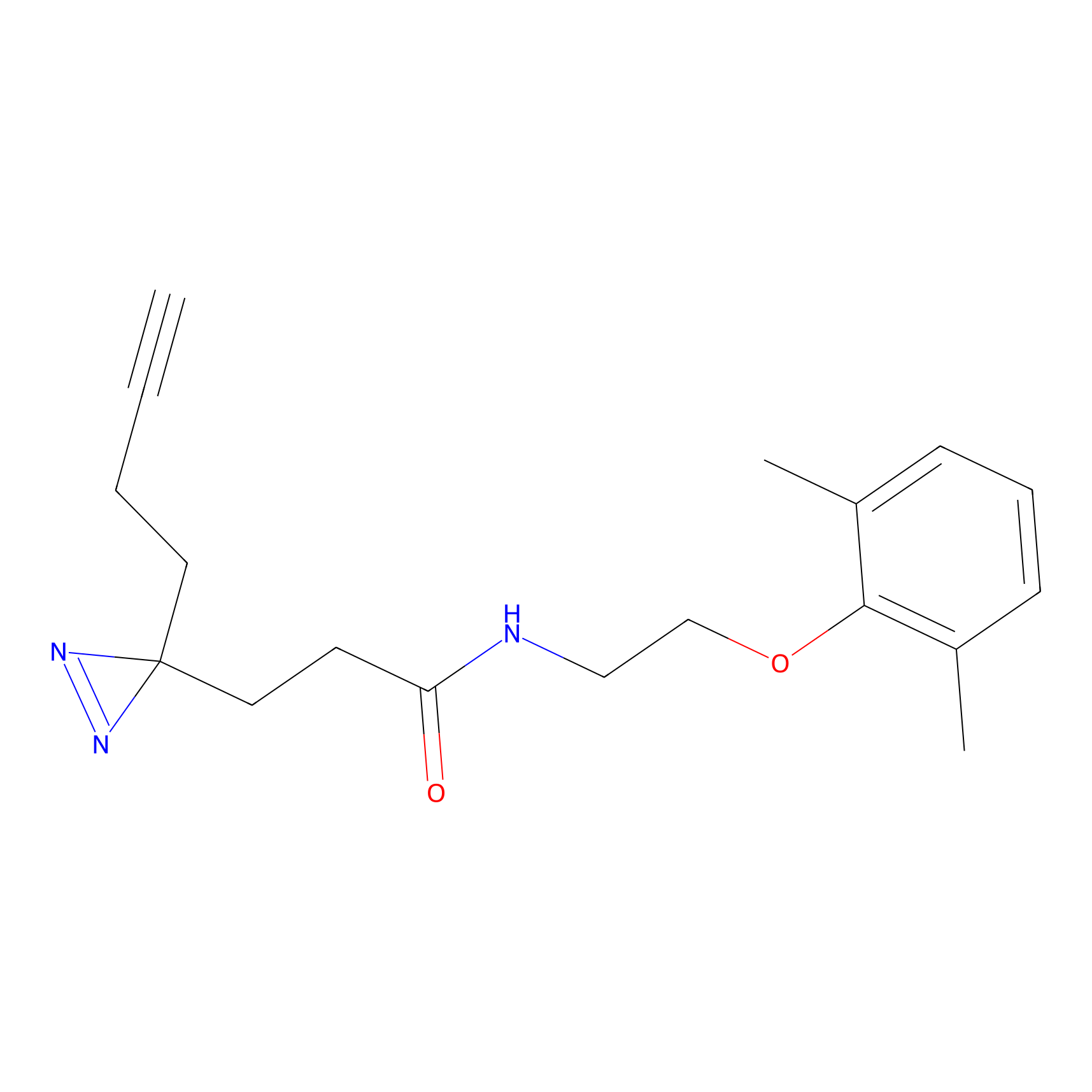
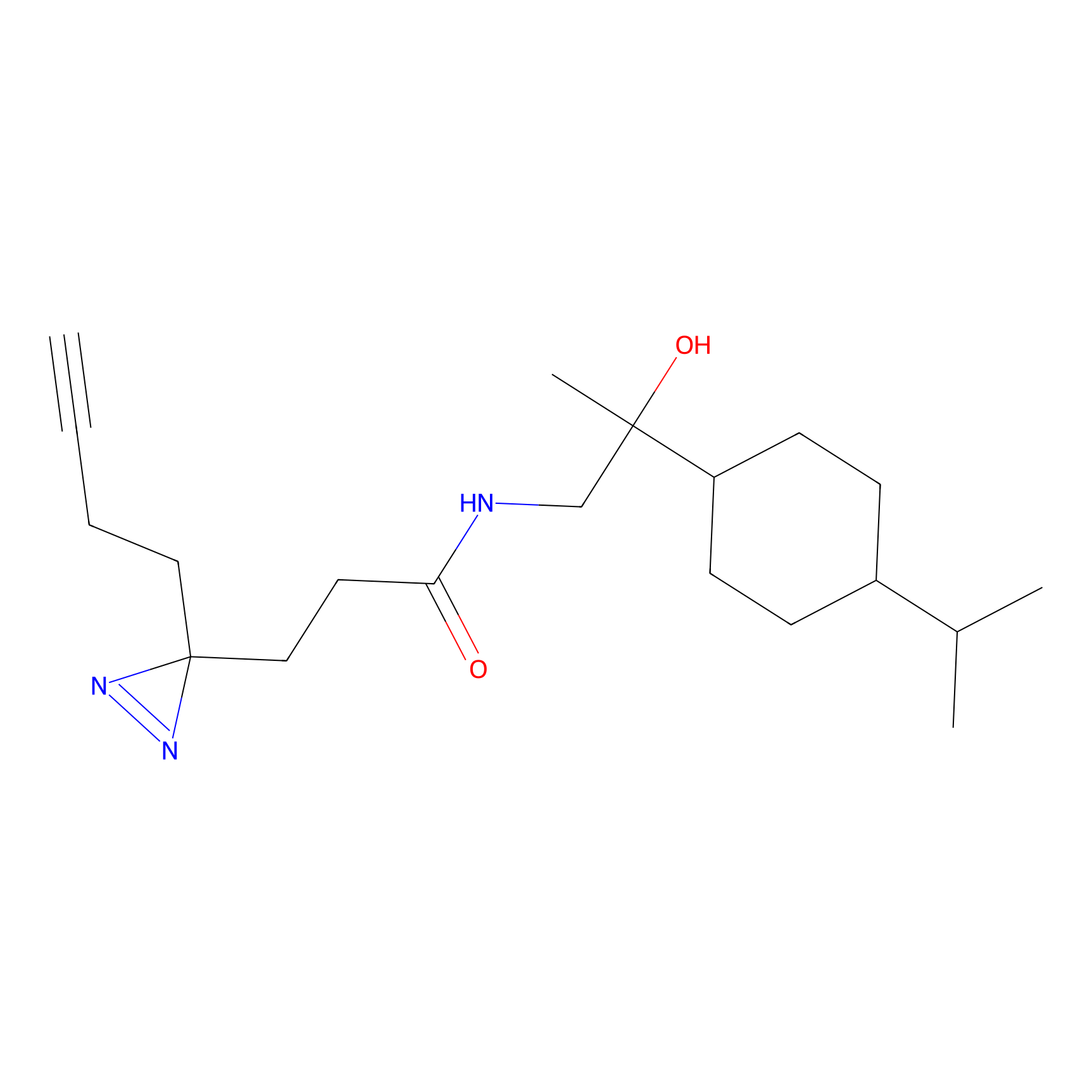
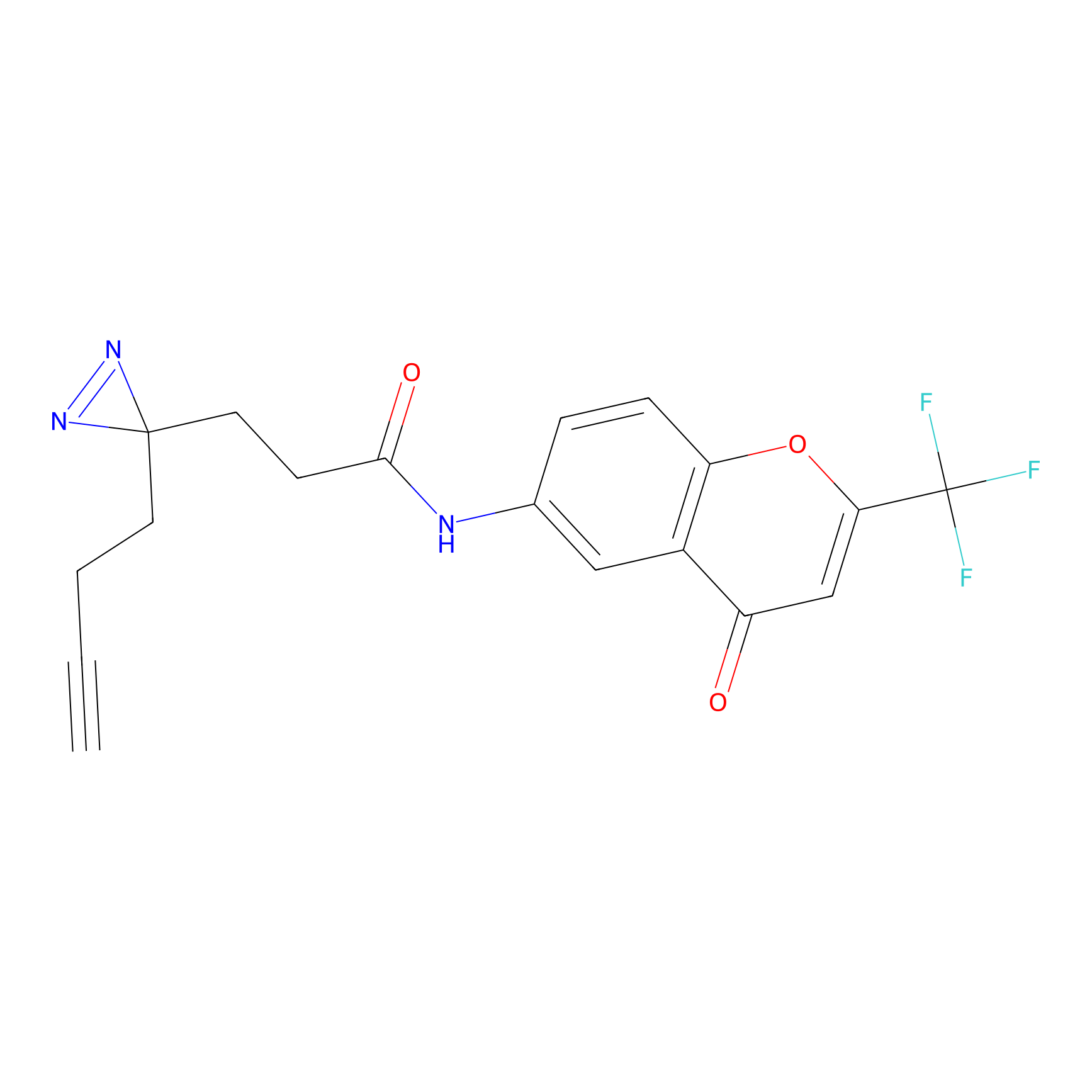
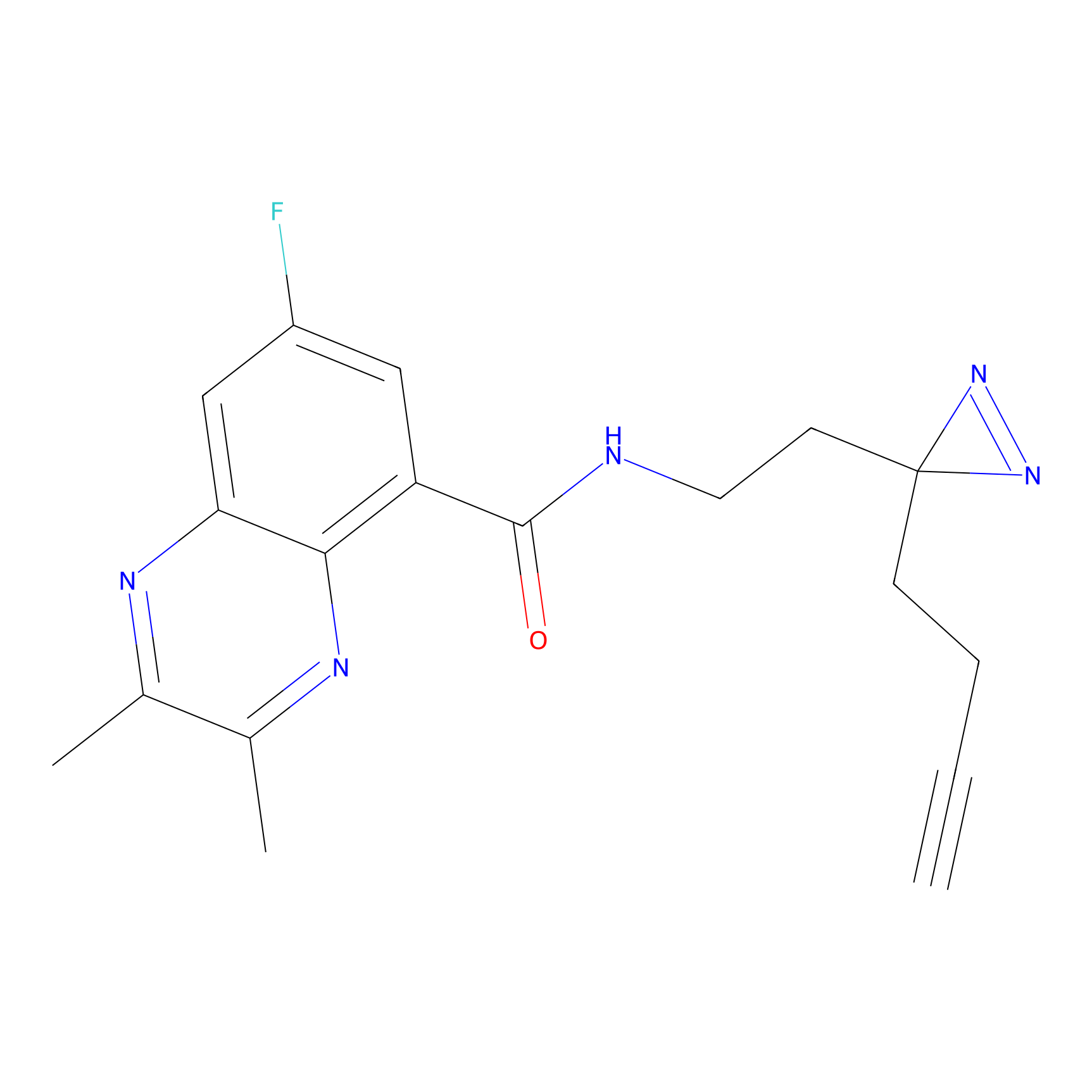
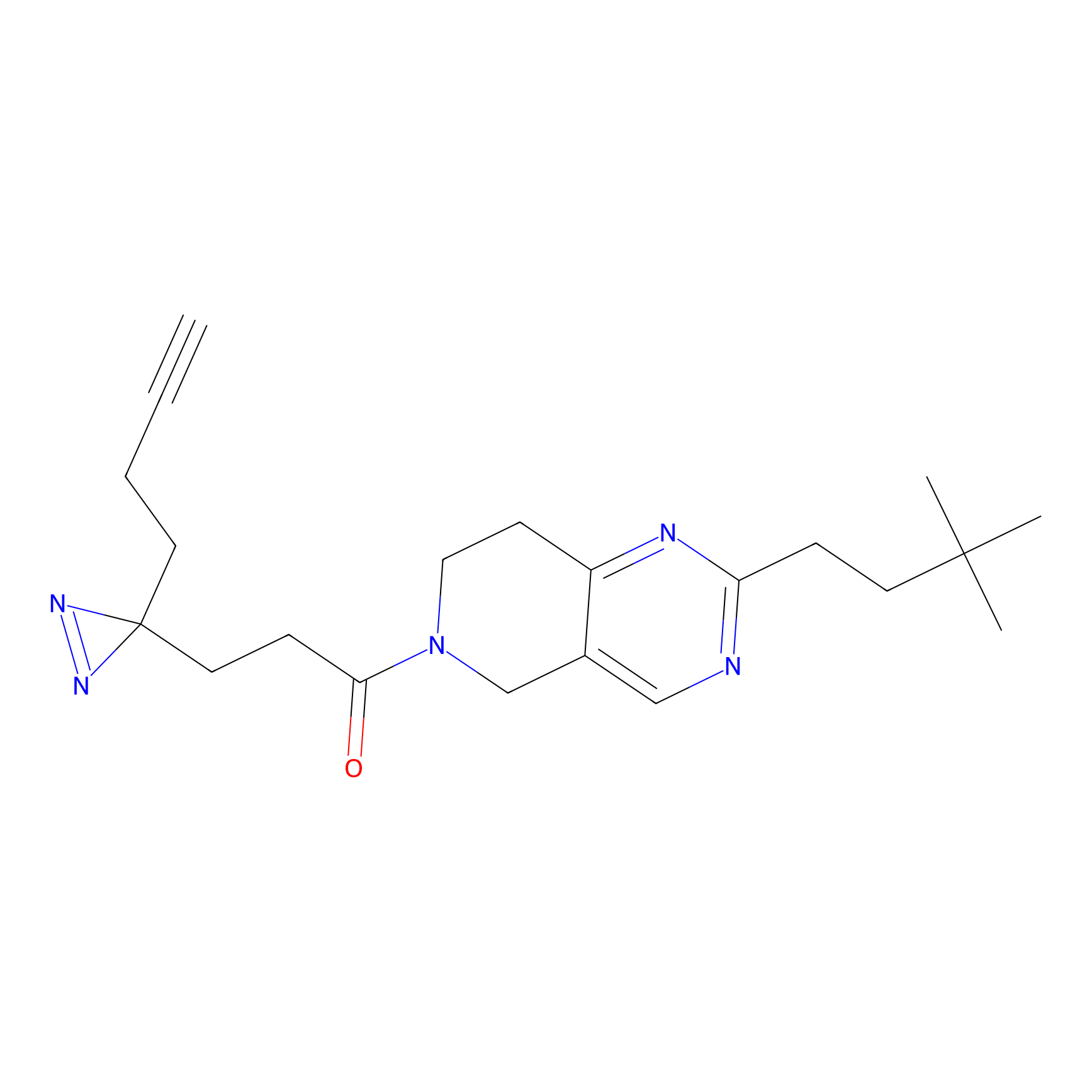
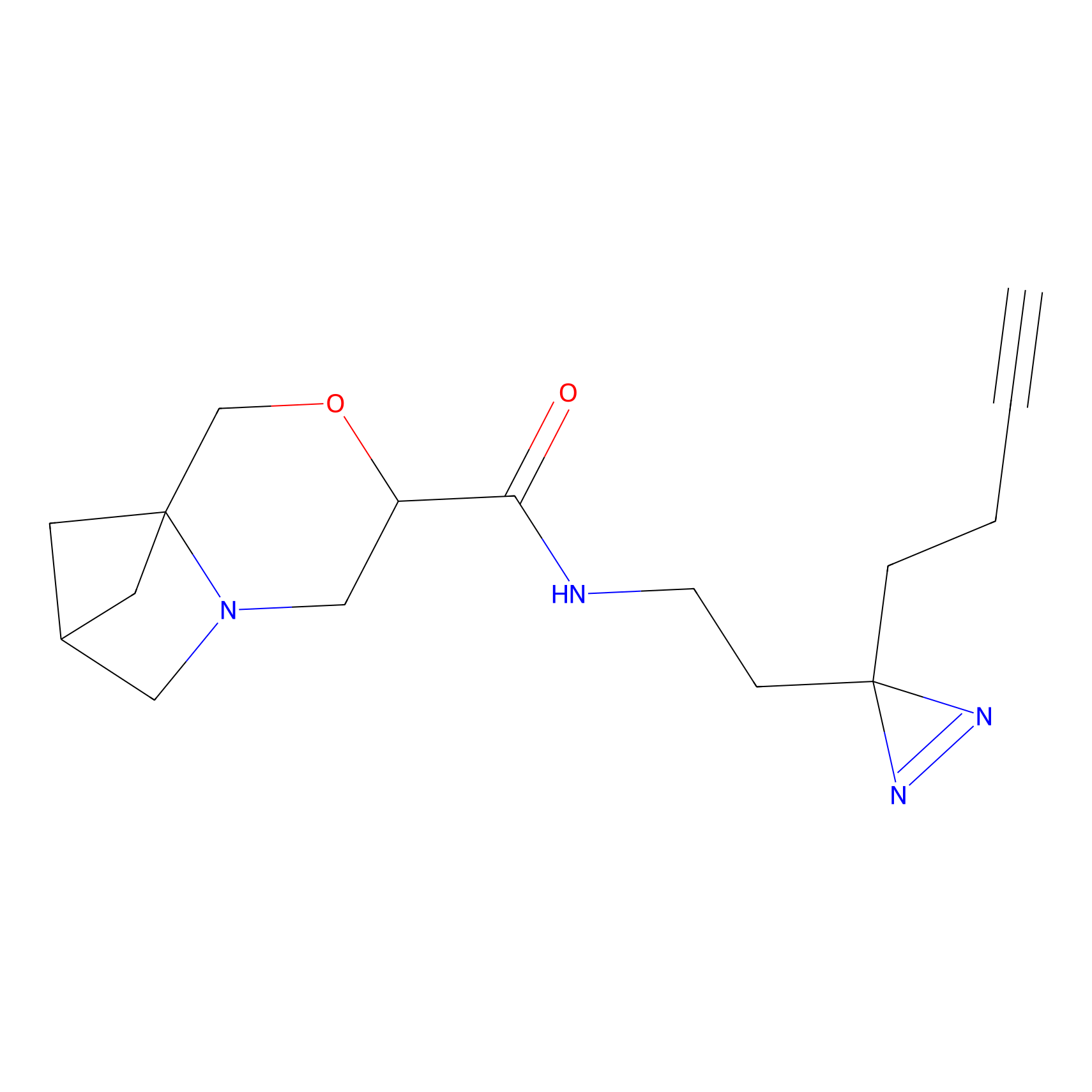
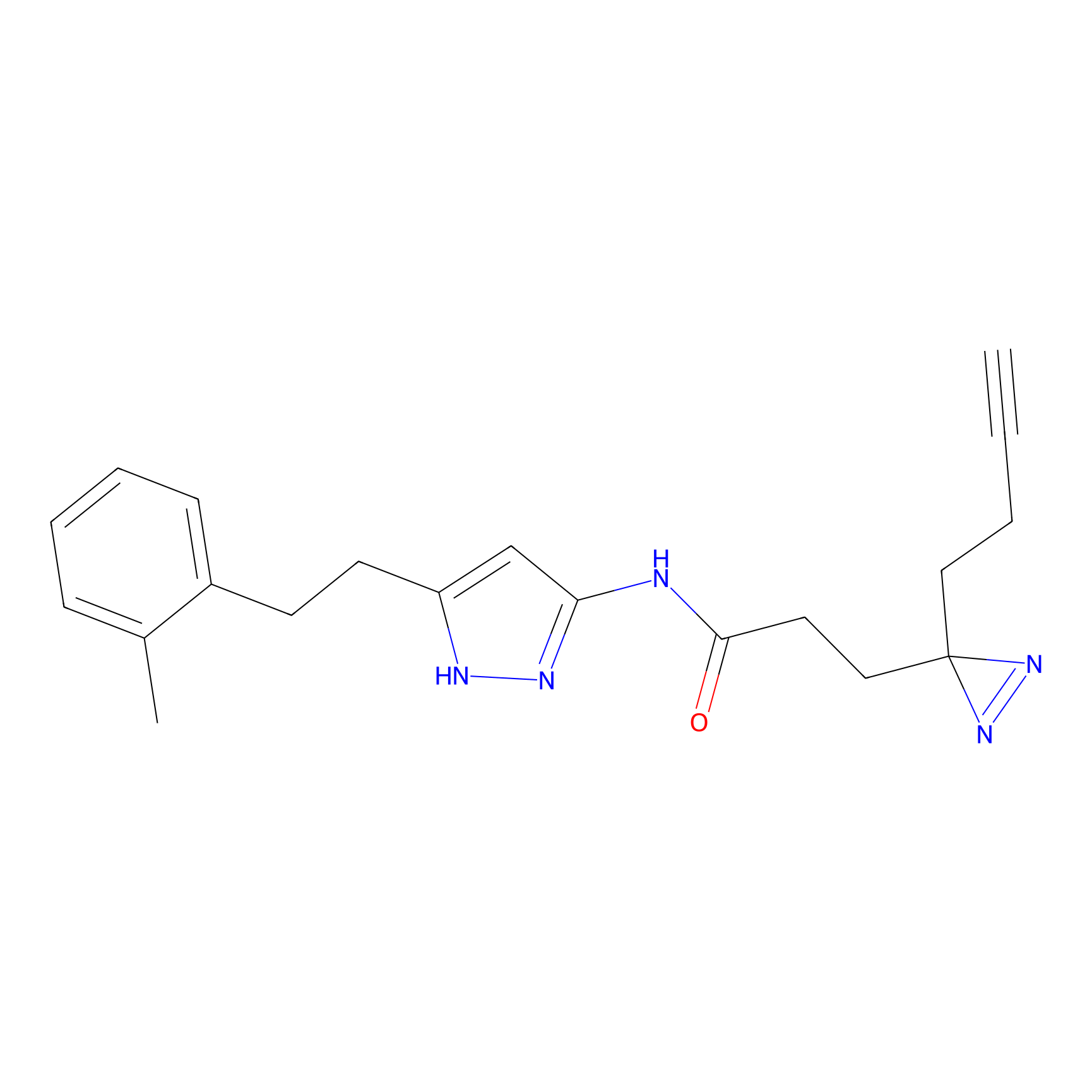
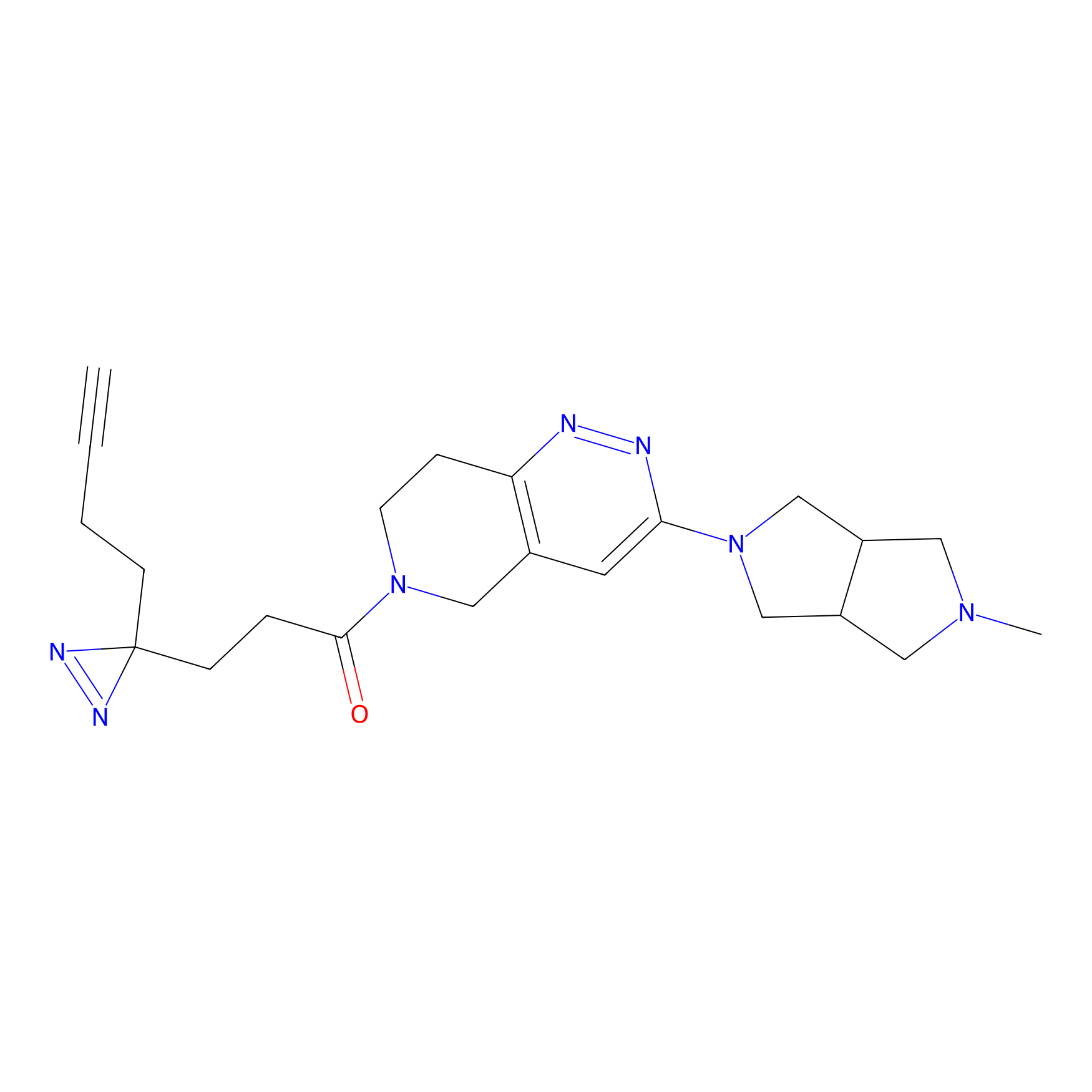
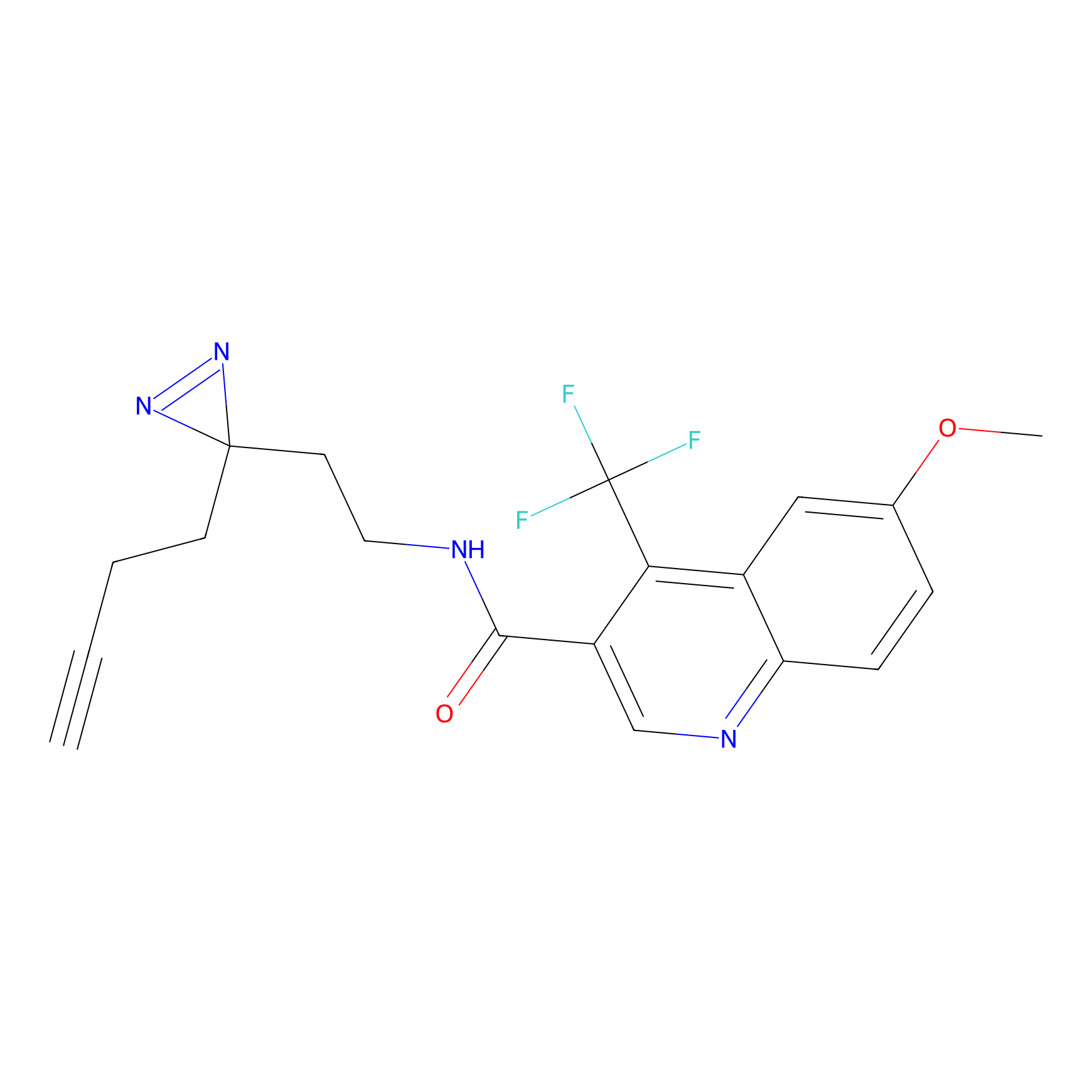
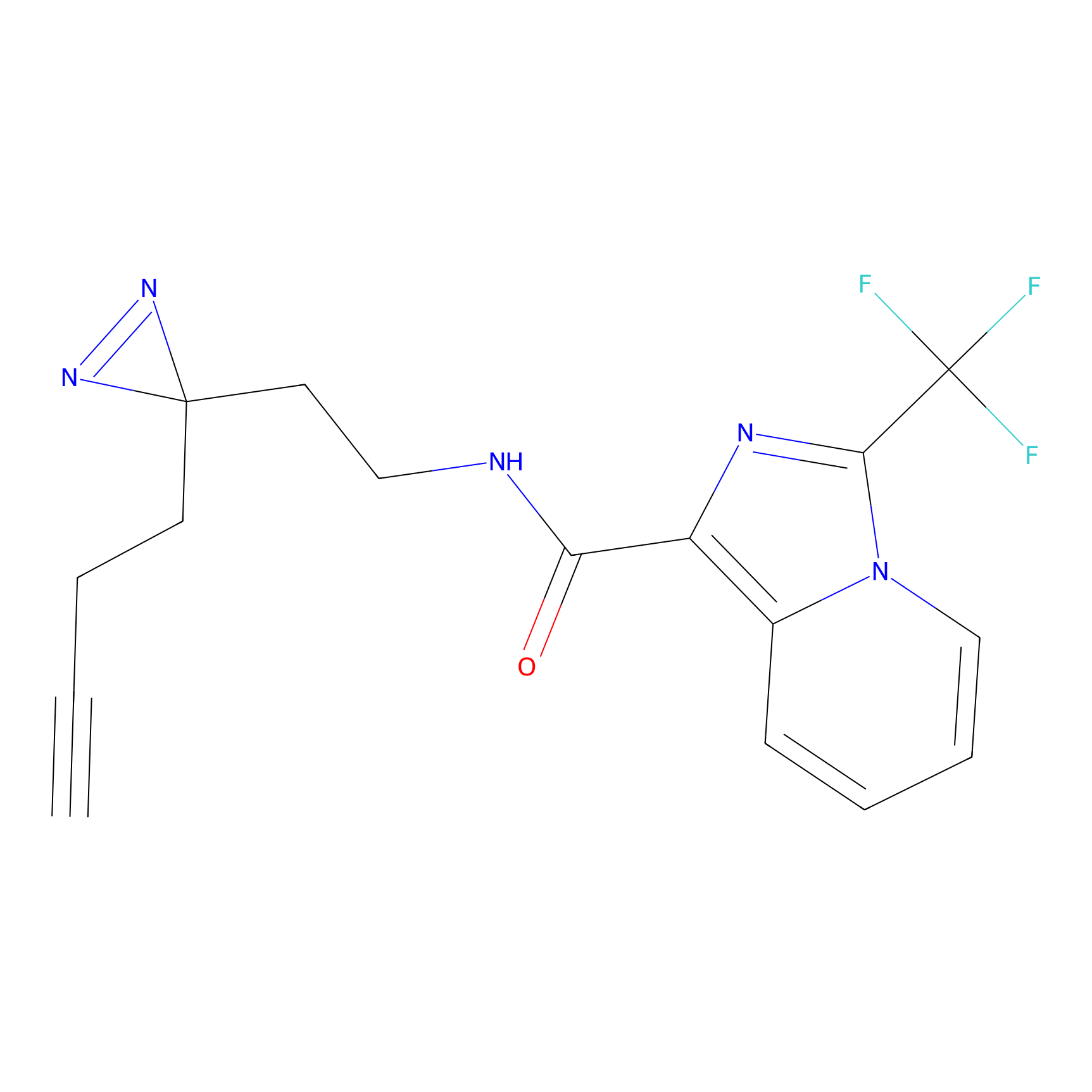
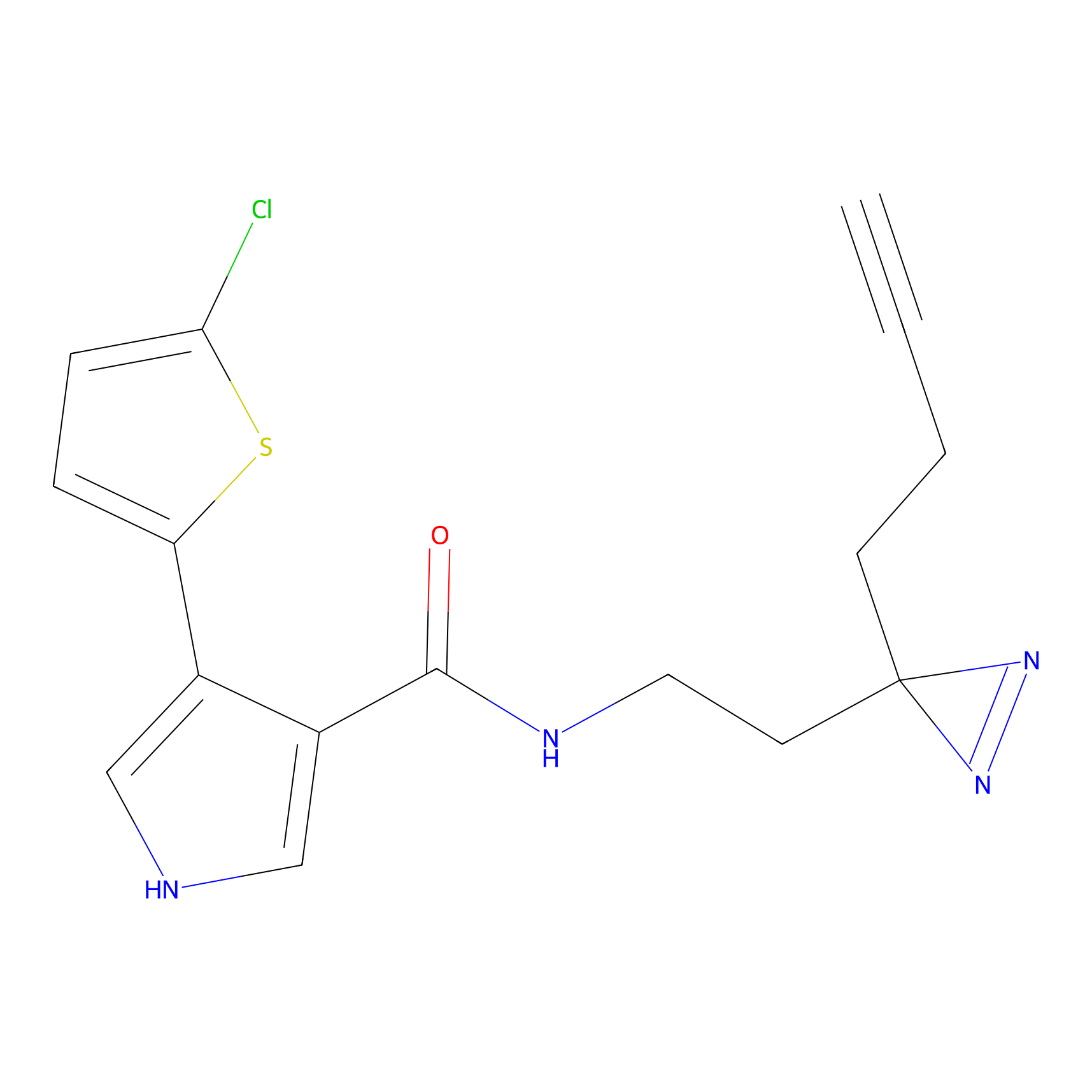
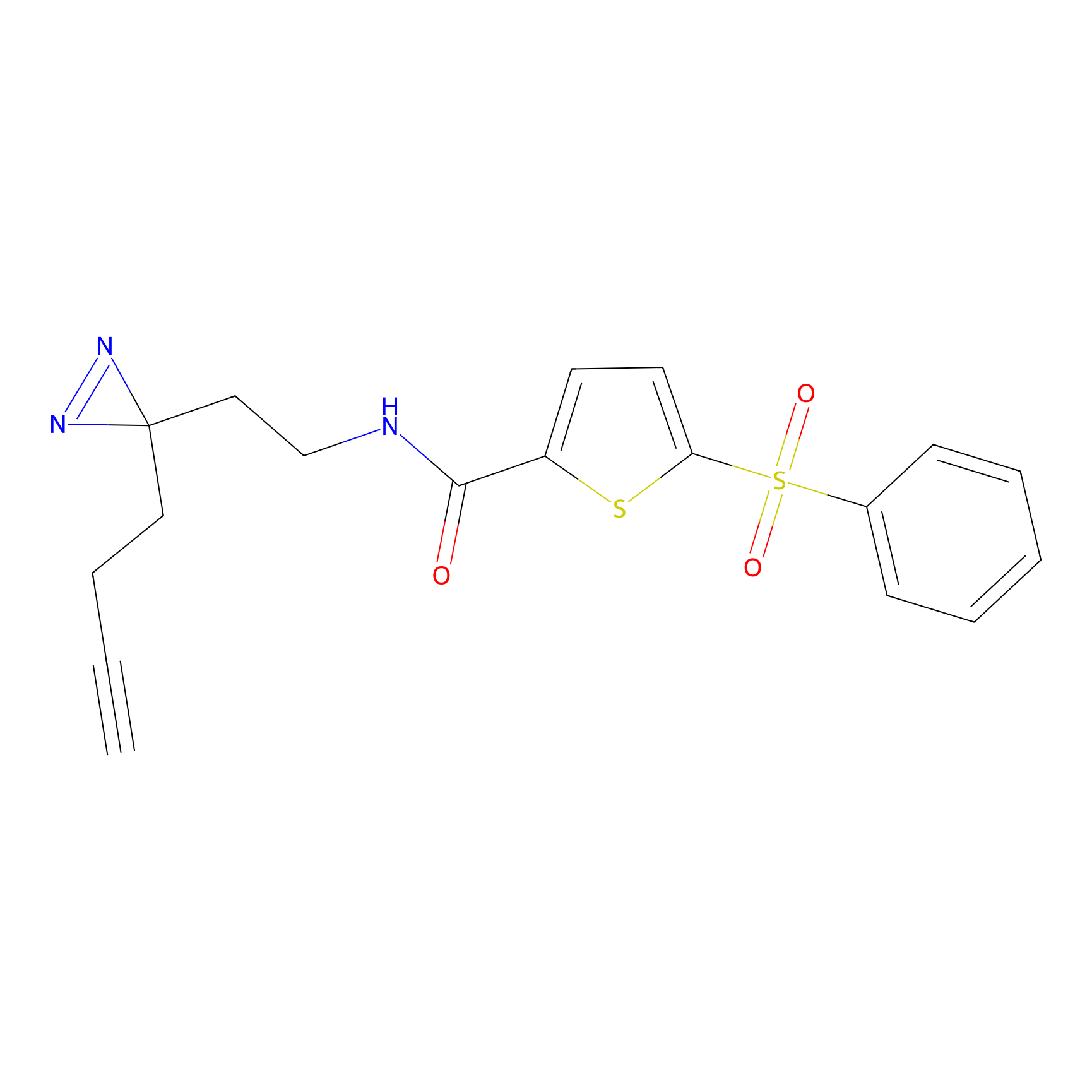
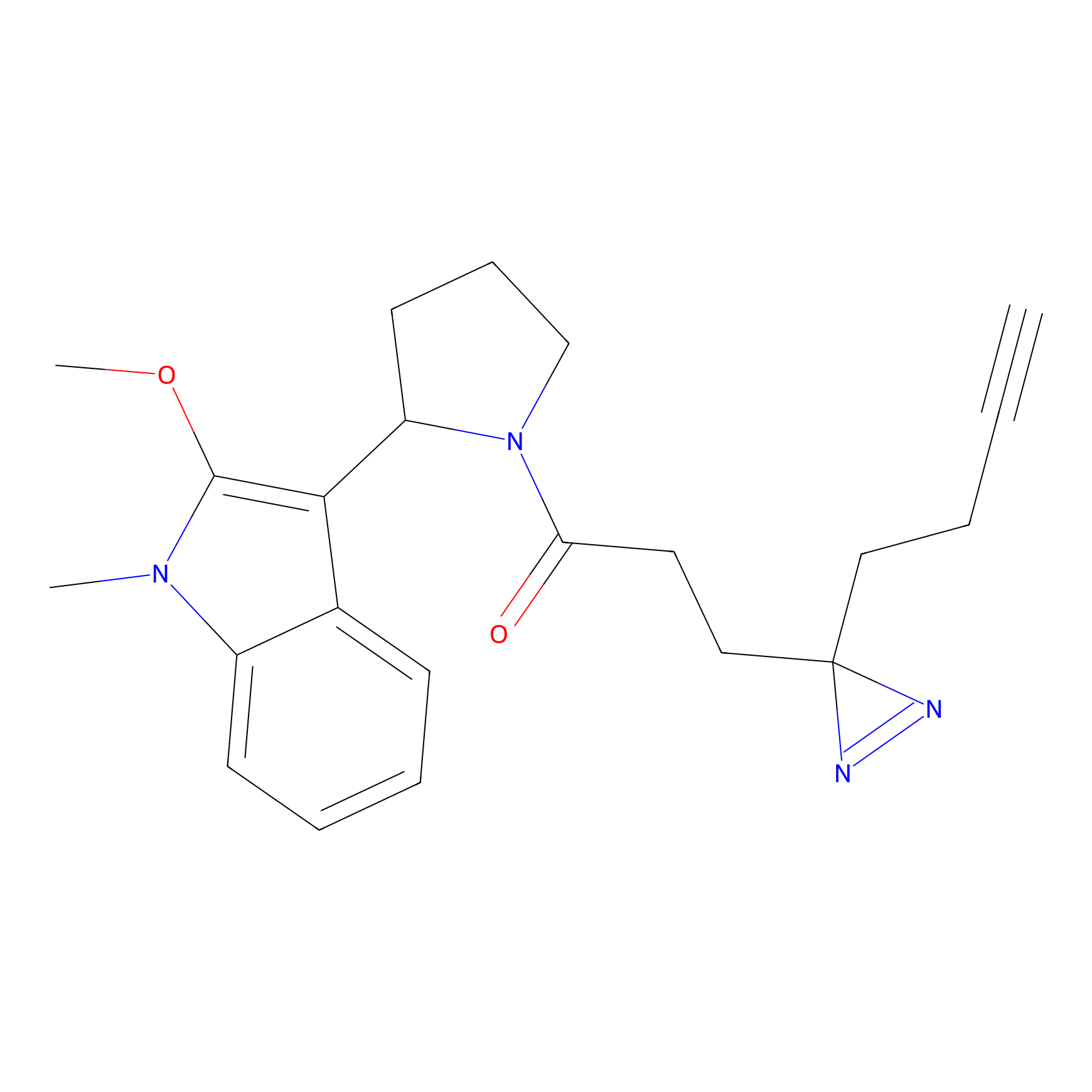
|
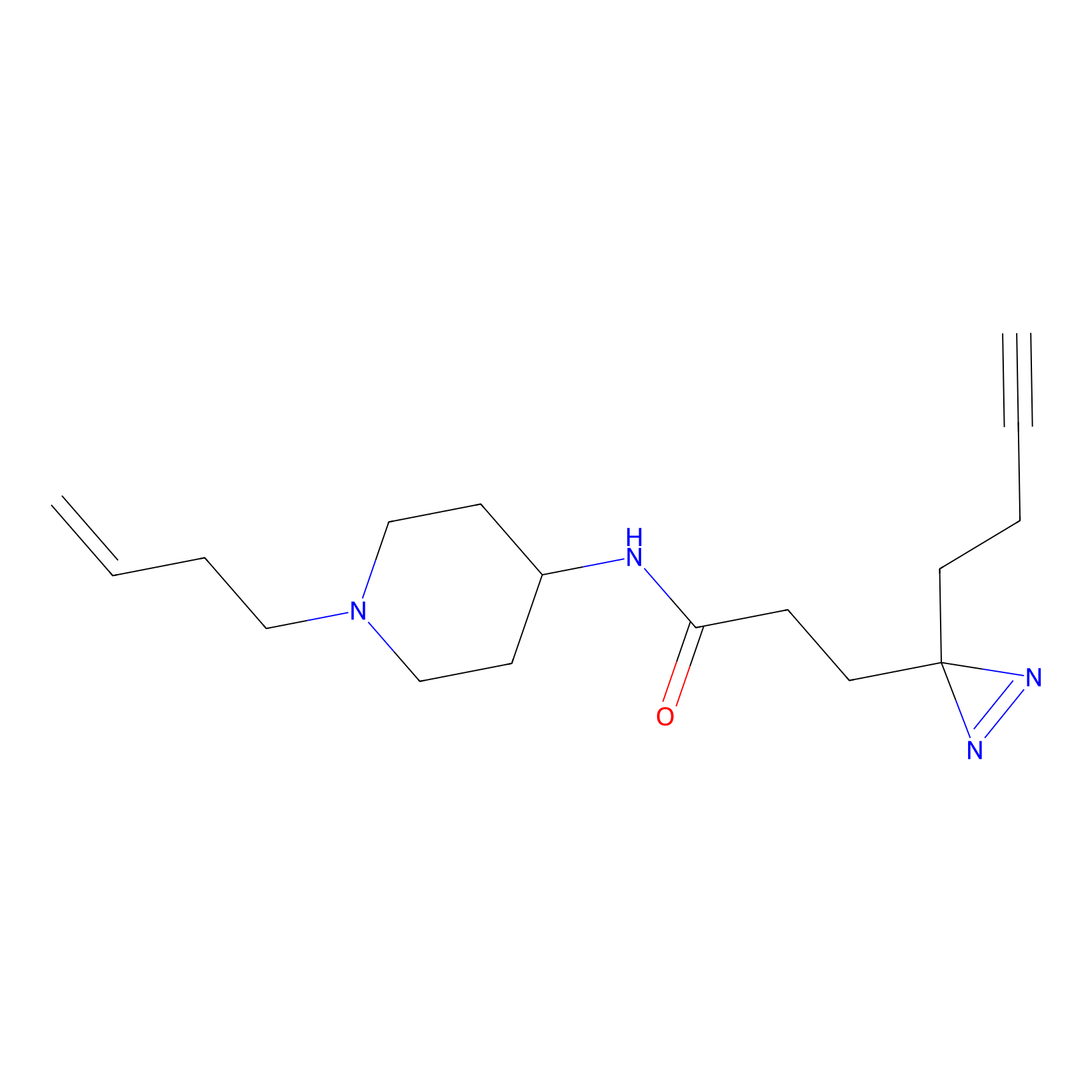
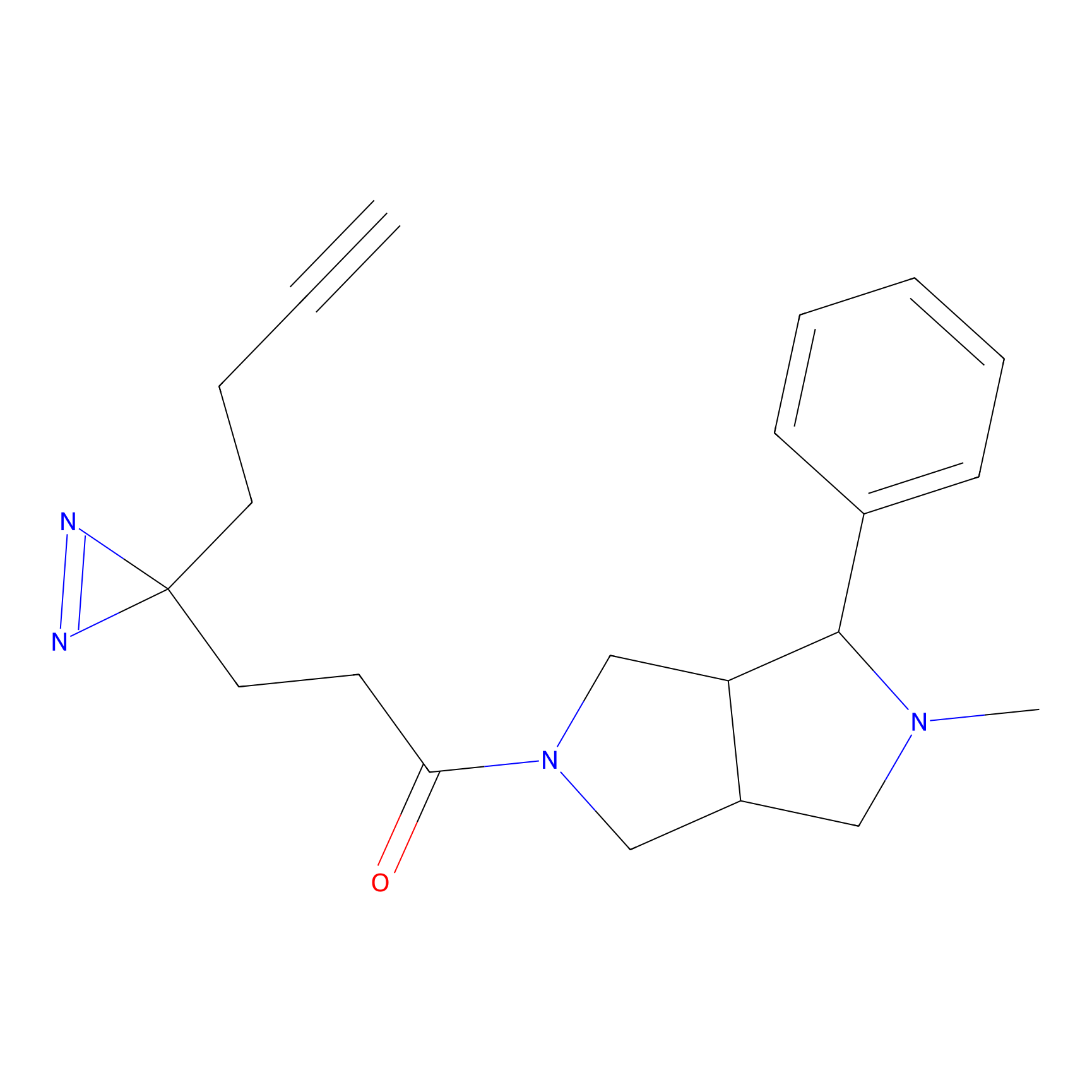
ONAyne Probe Info |
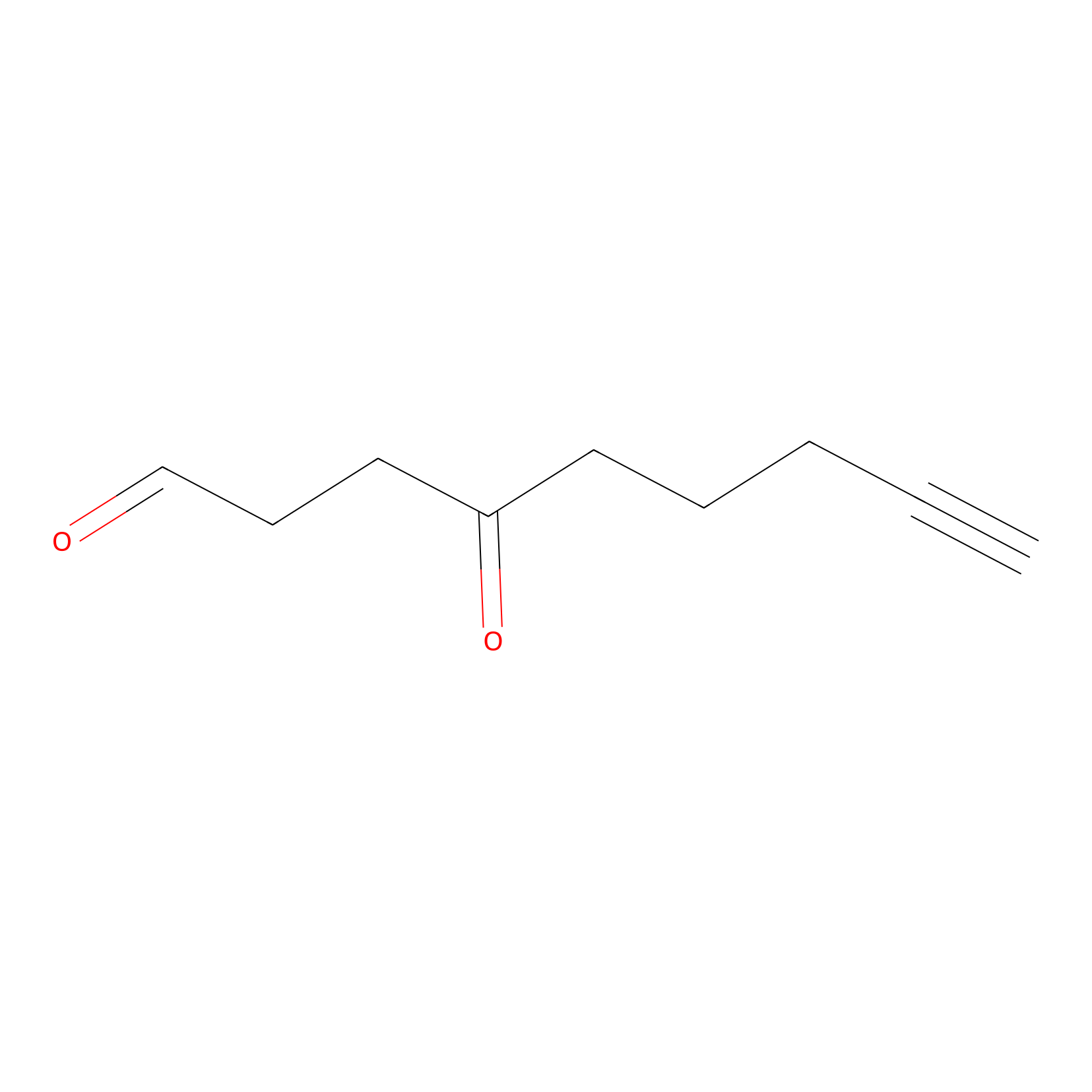 |
K239(10.00) | LDD0275 | [2] | |
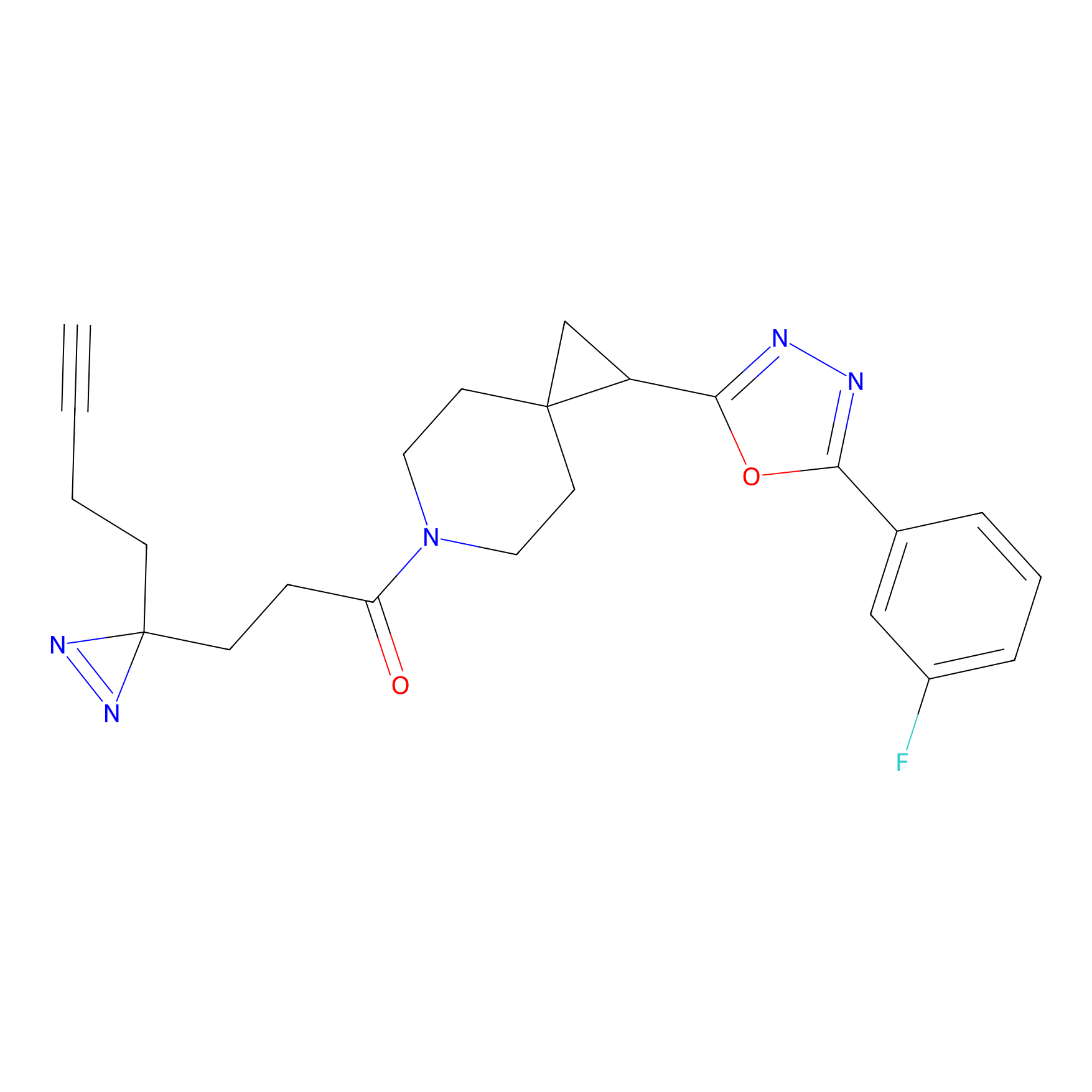
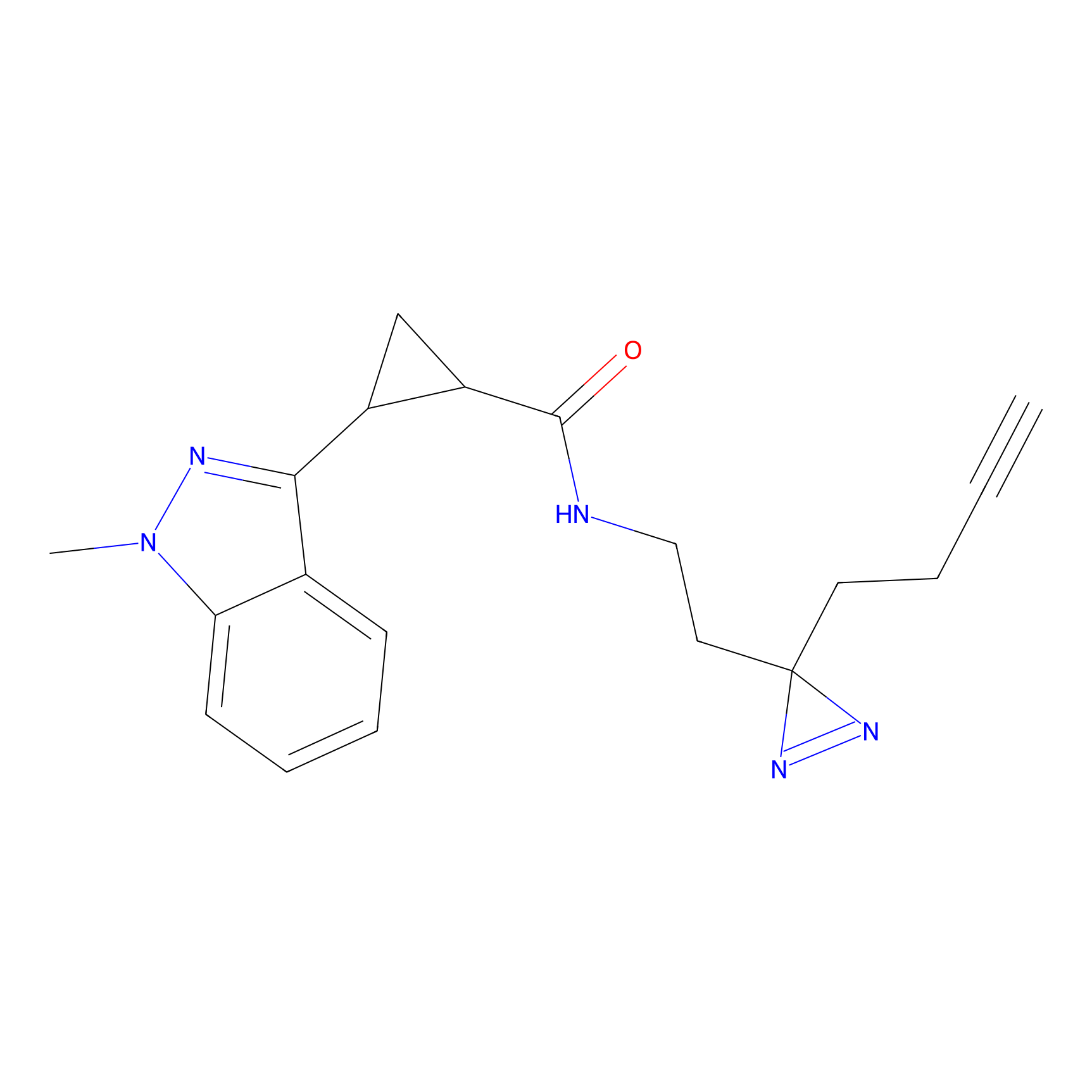
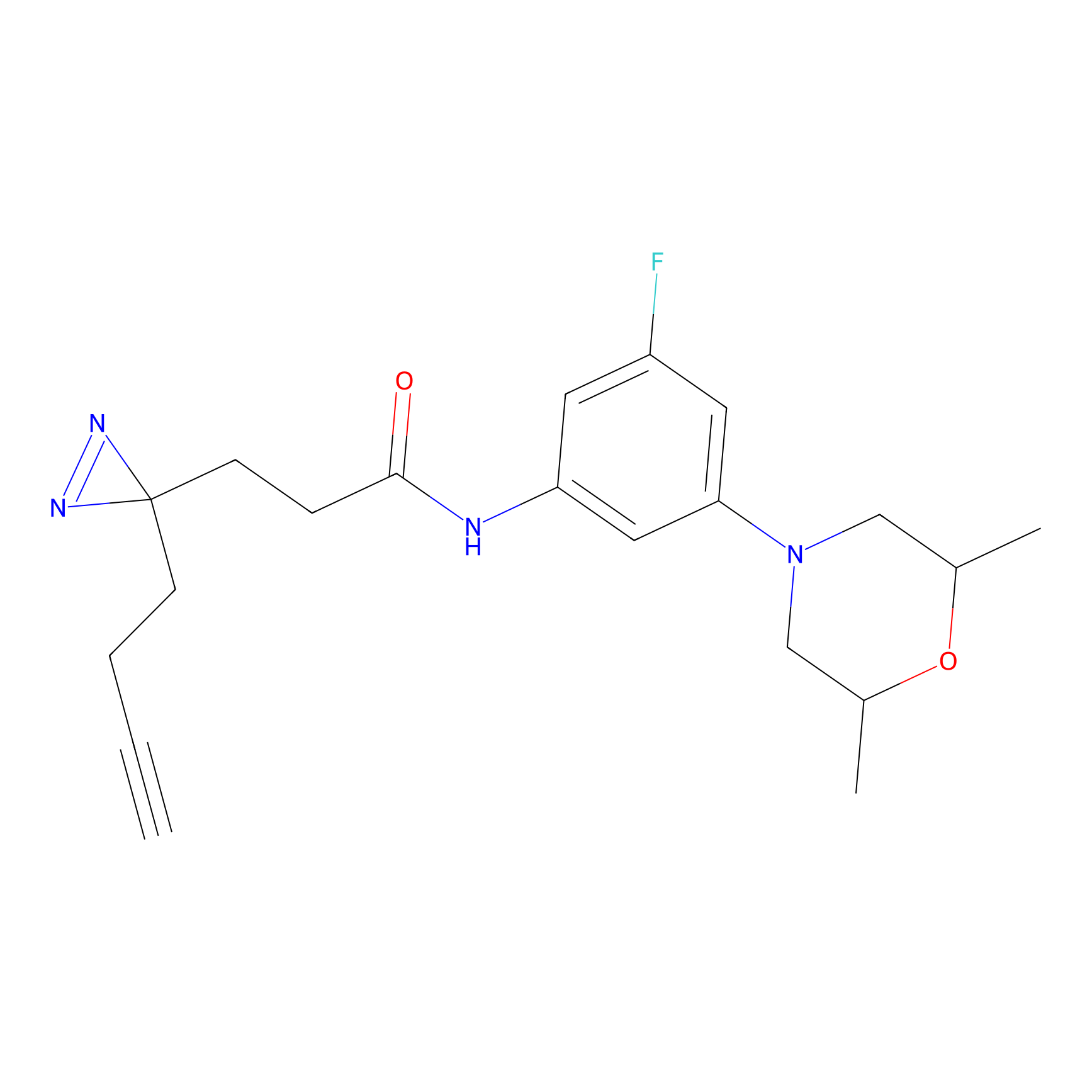
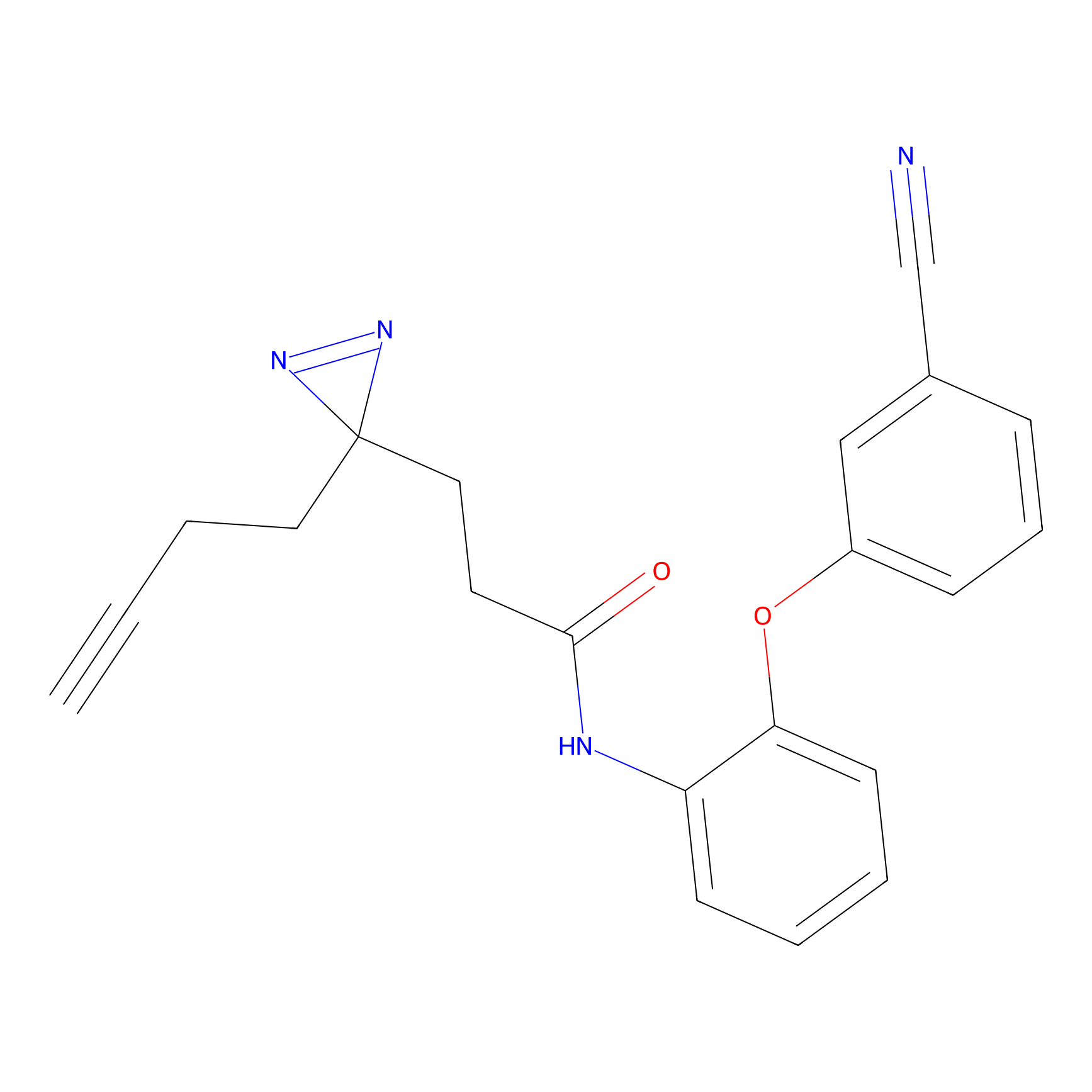
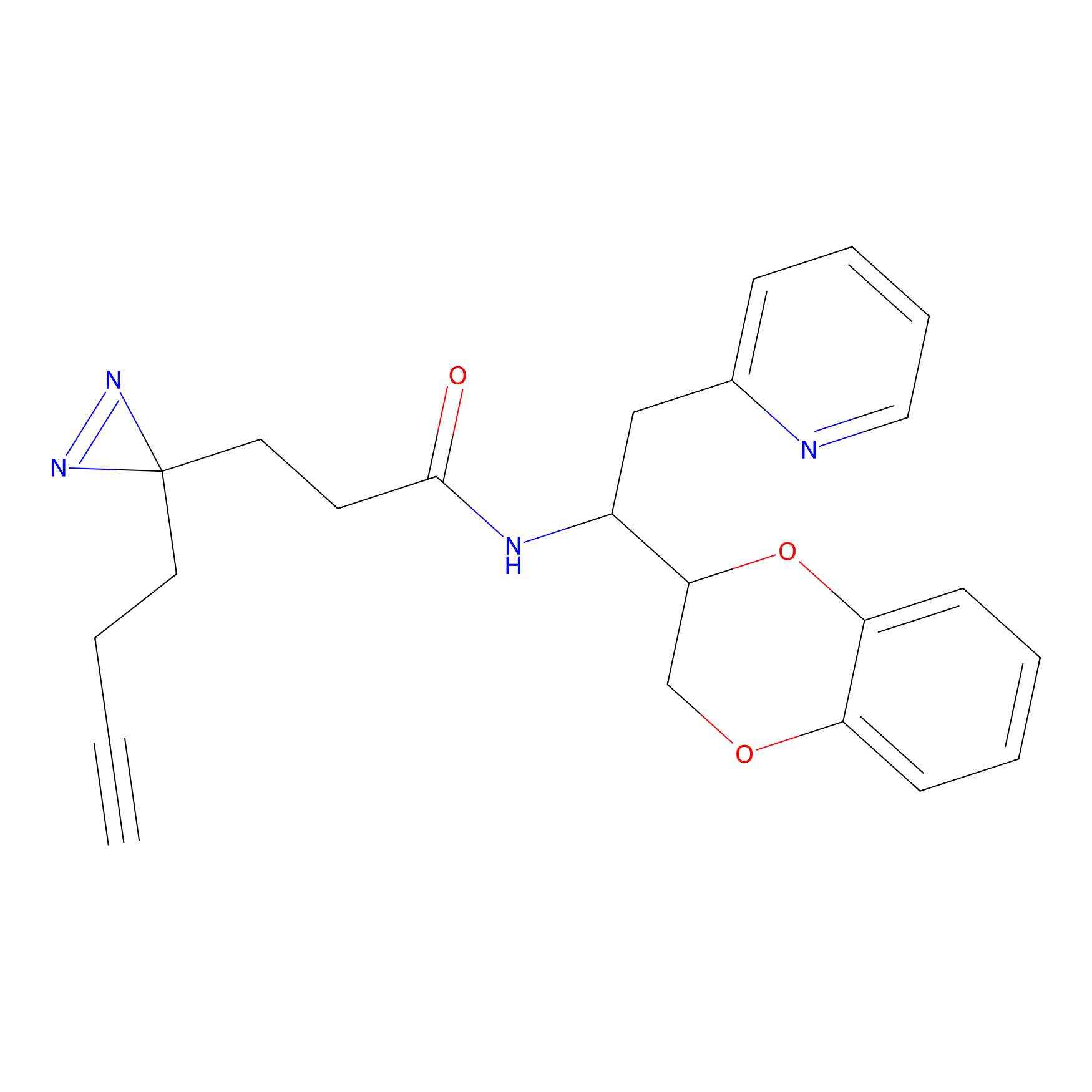
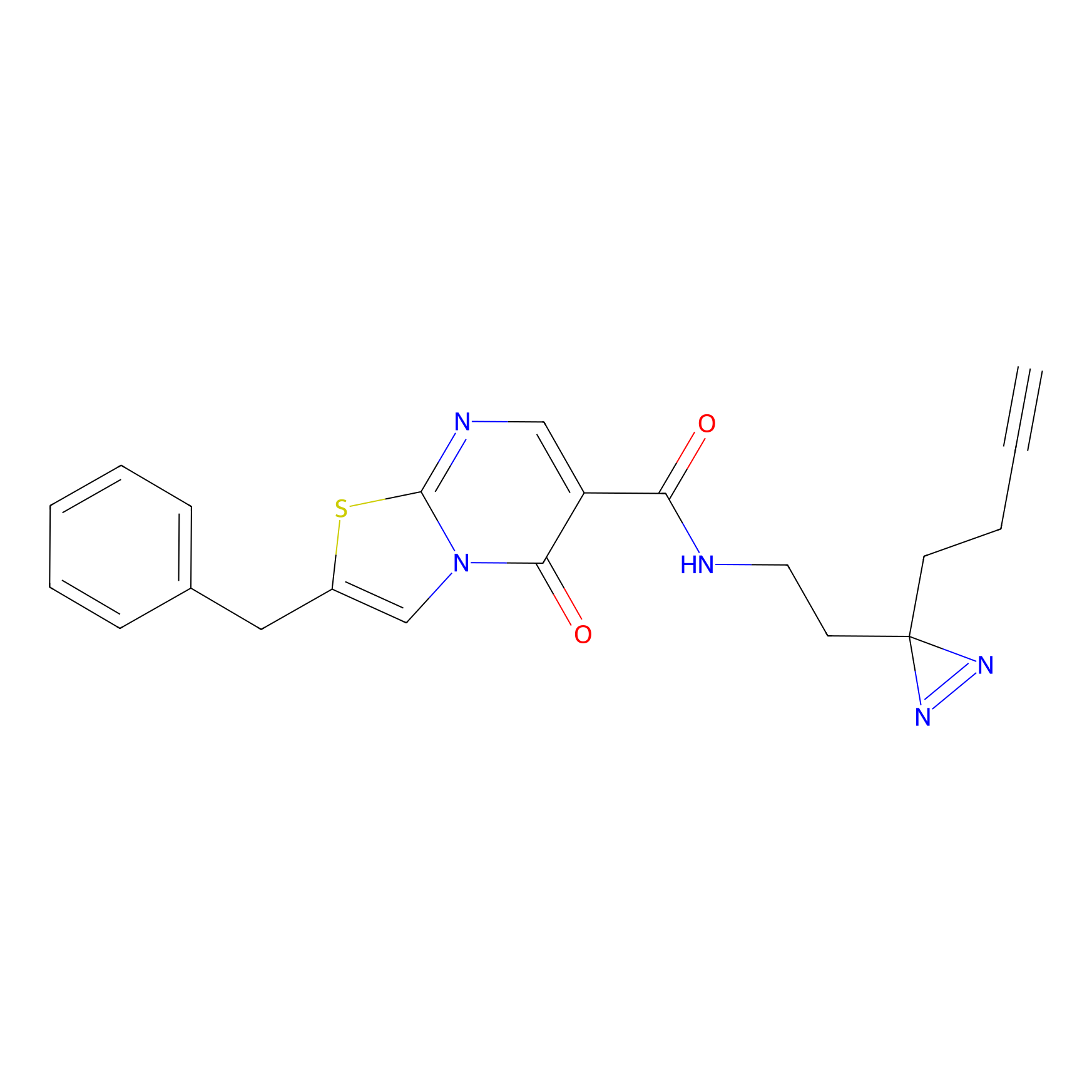
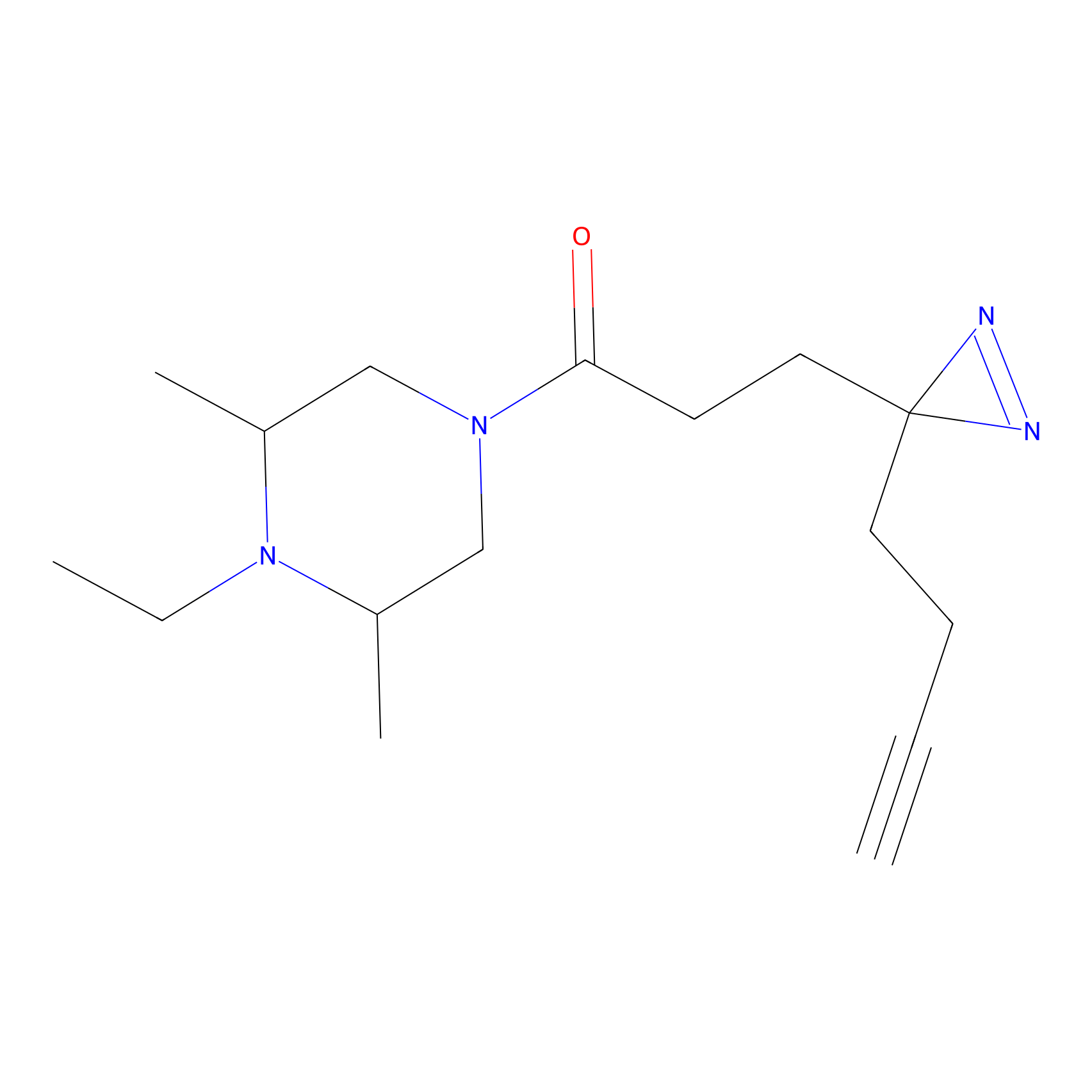
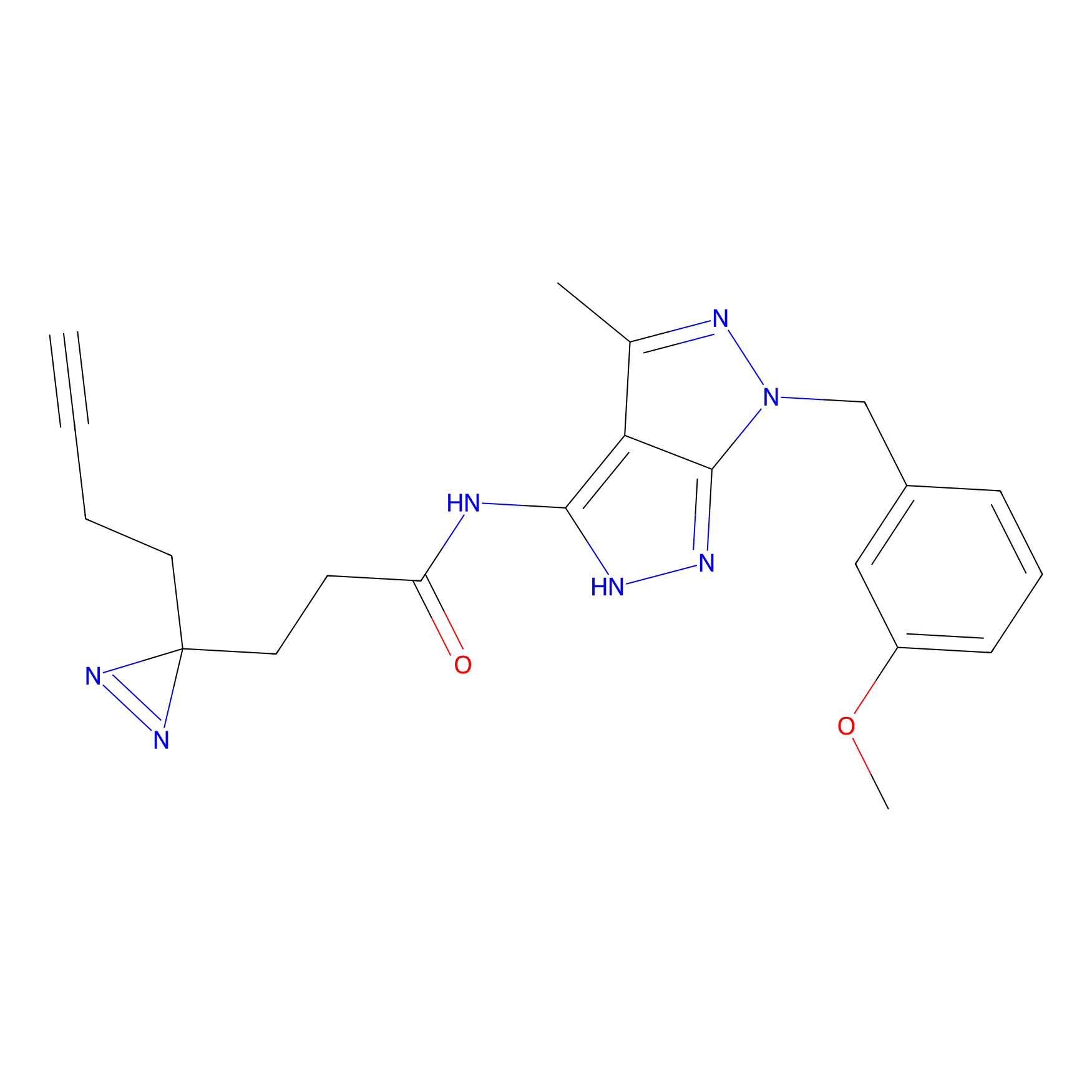
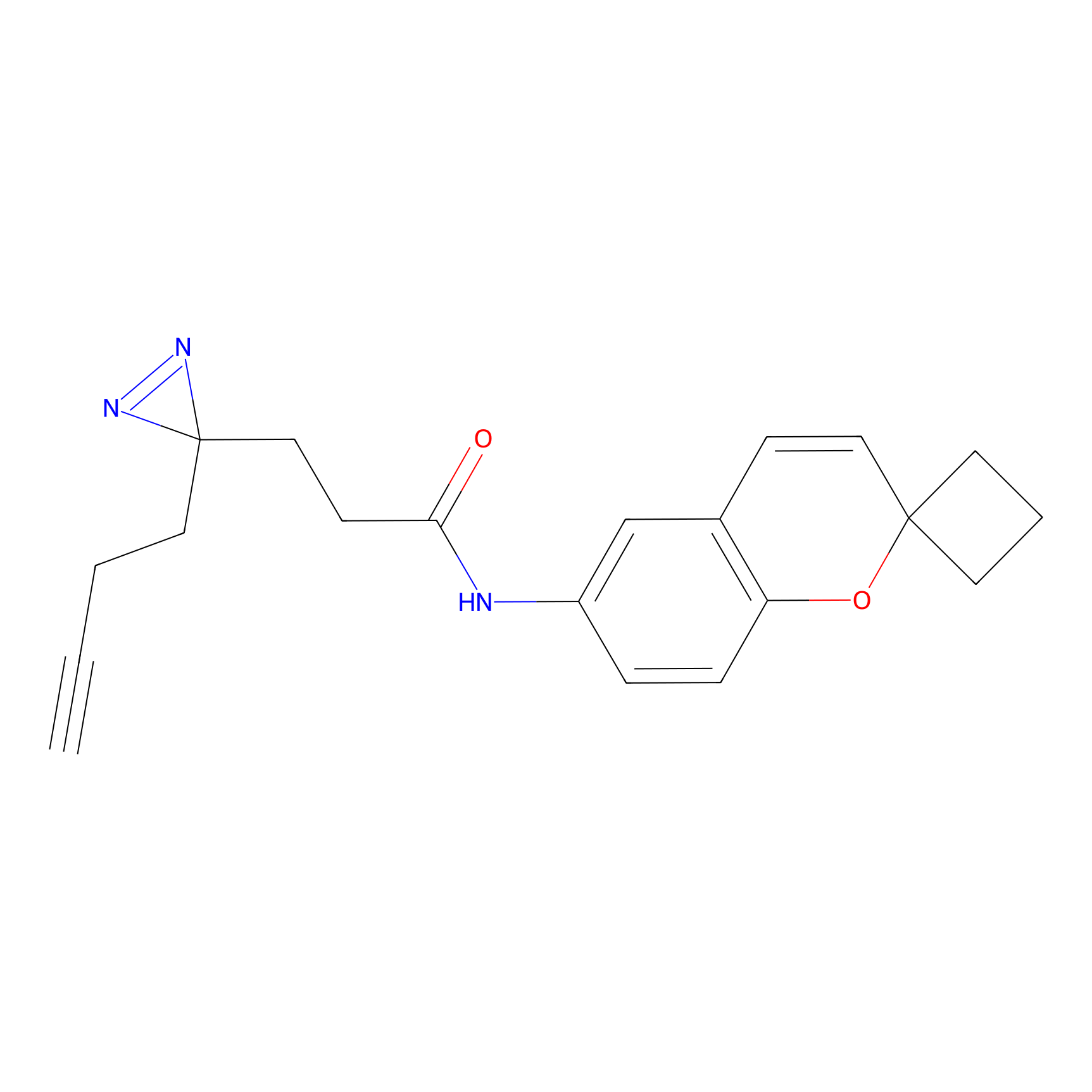
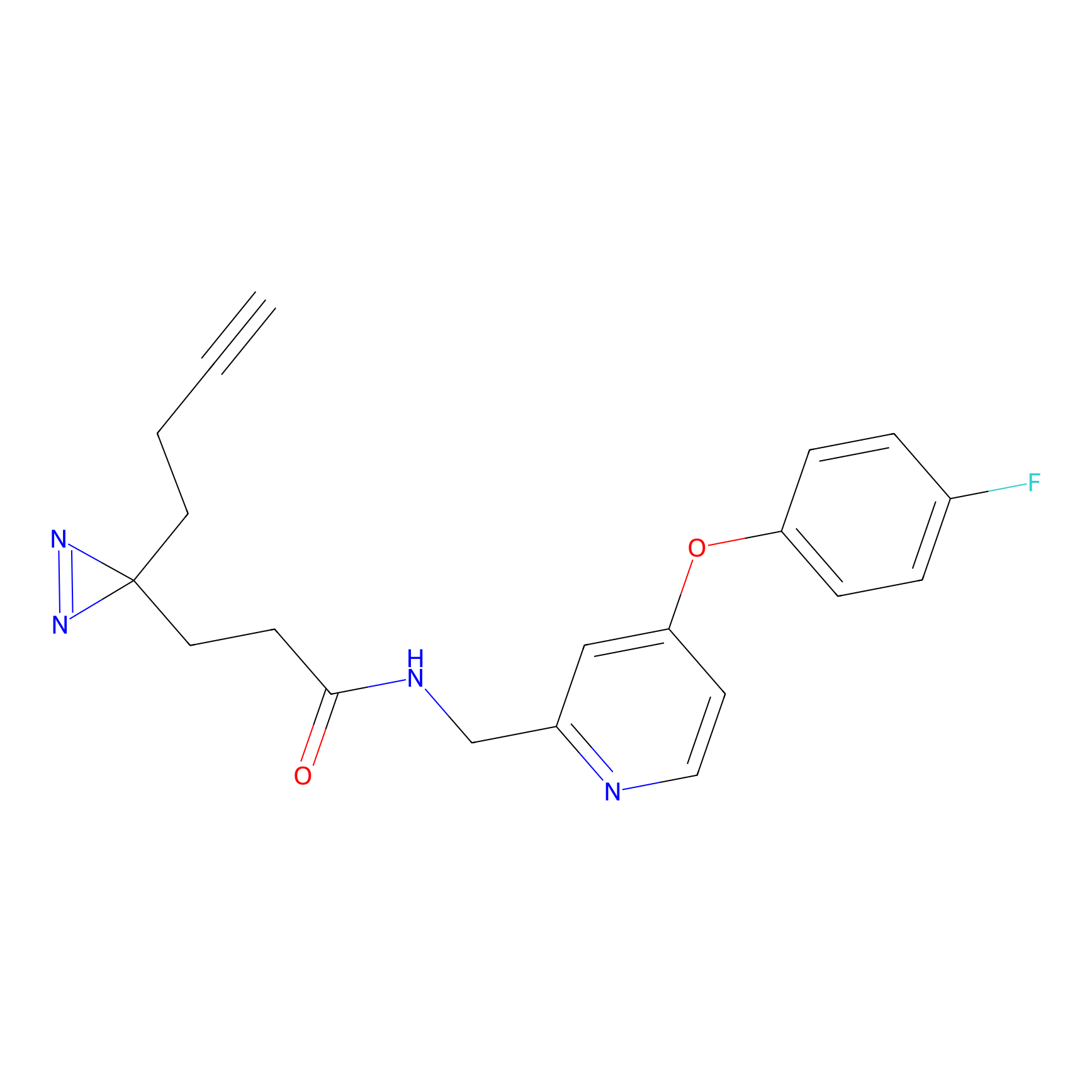
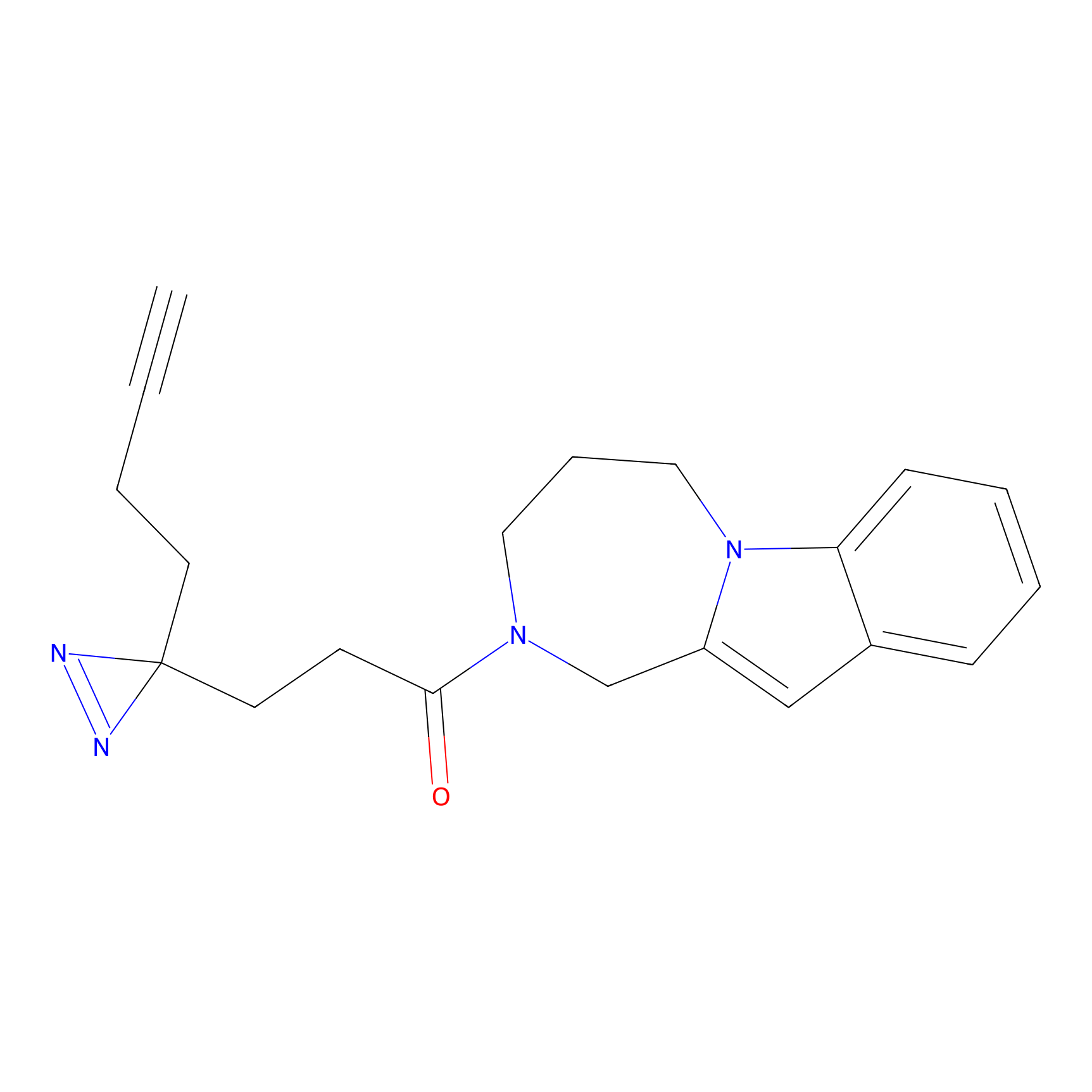
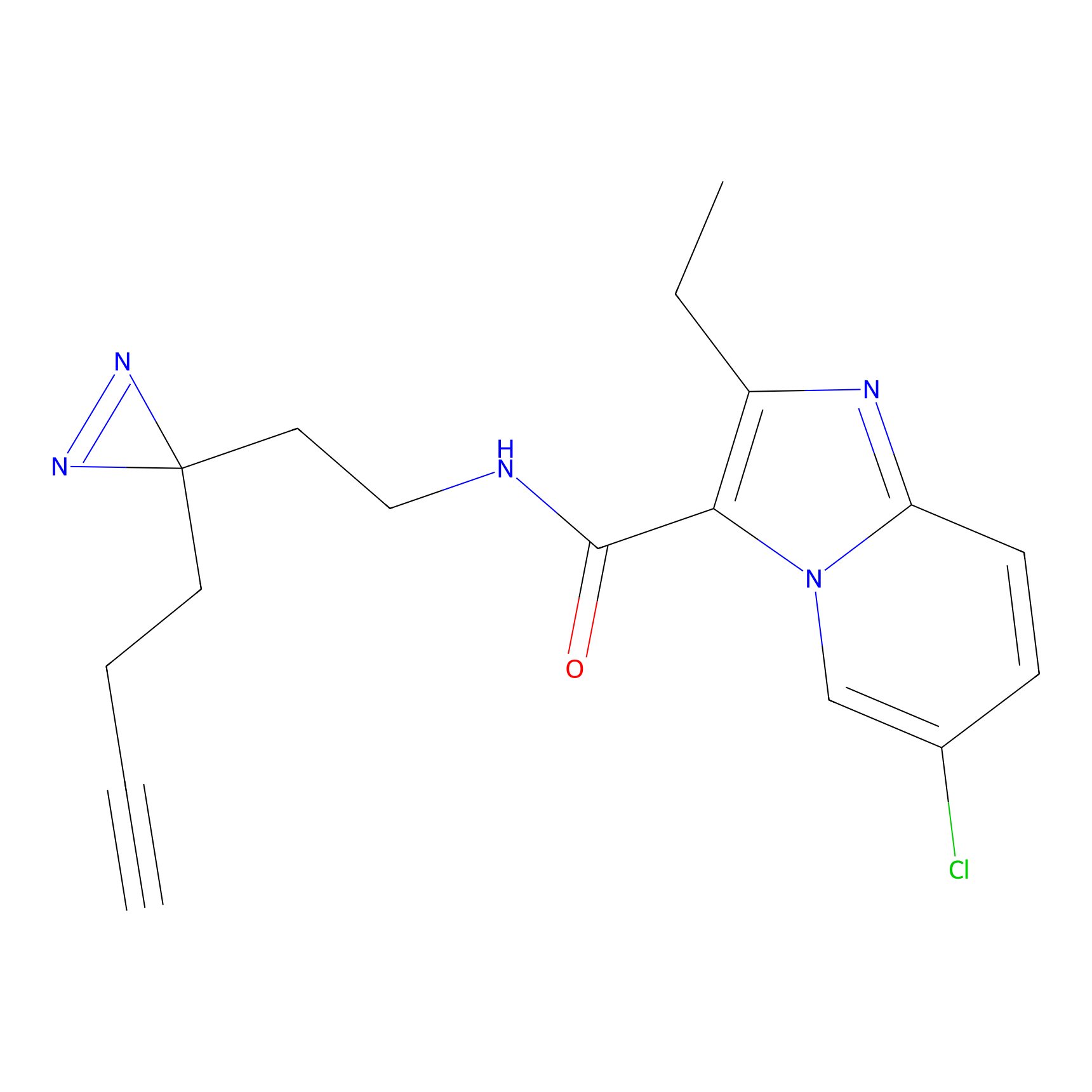
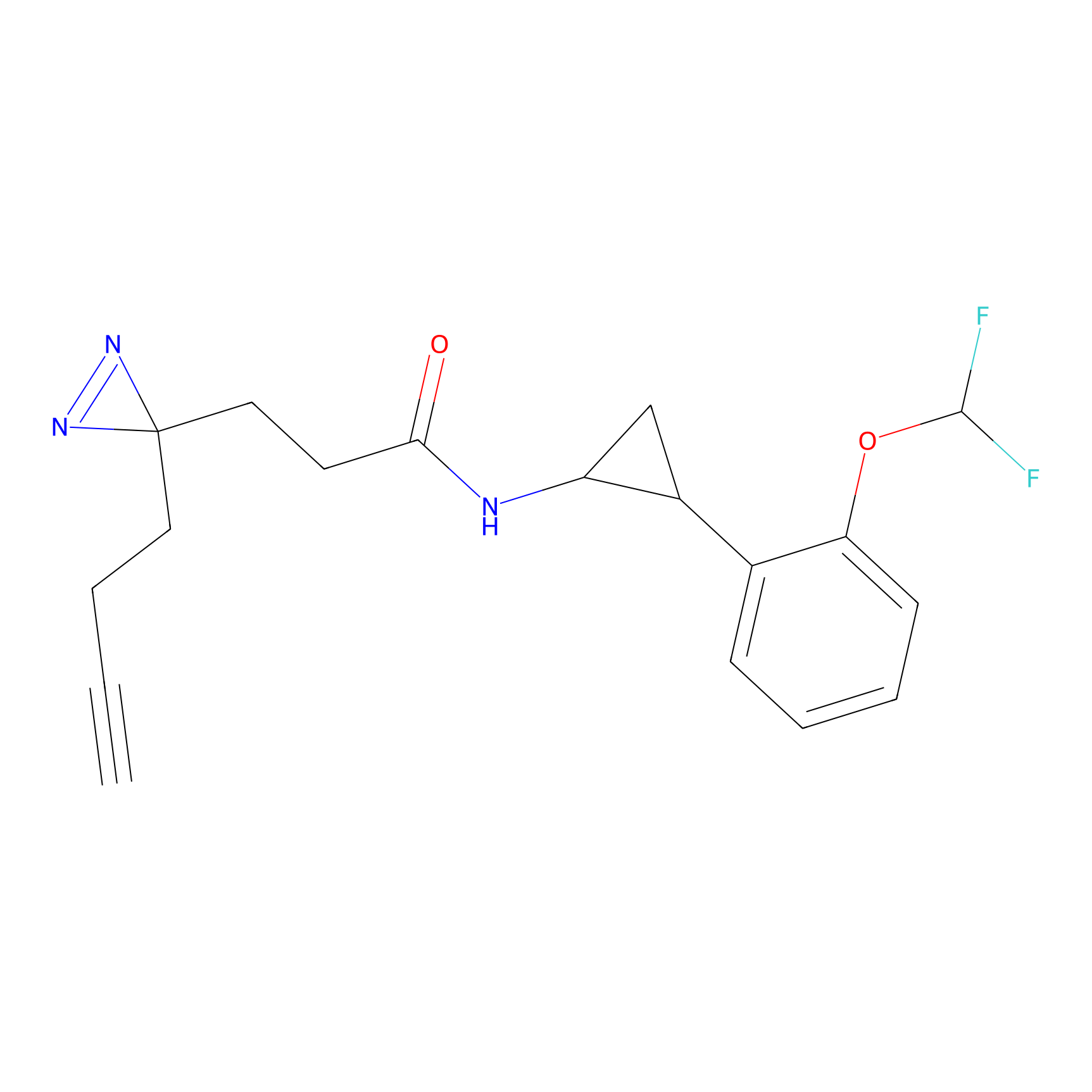
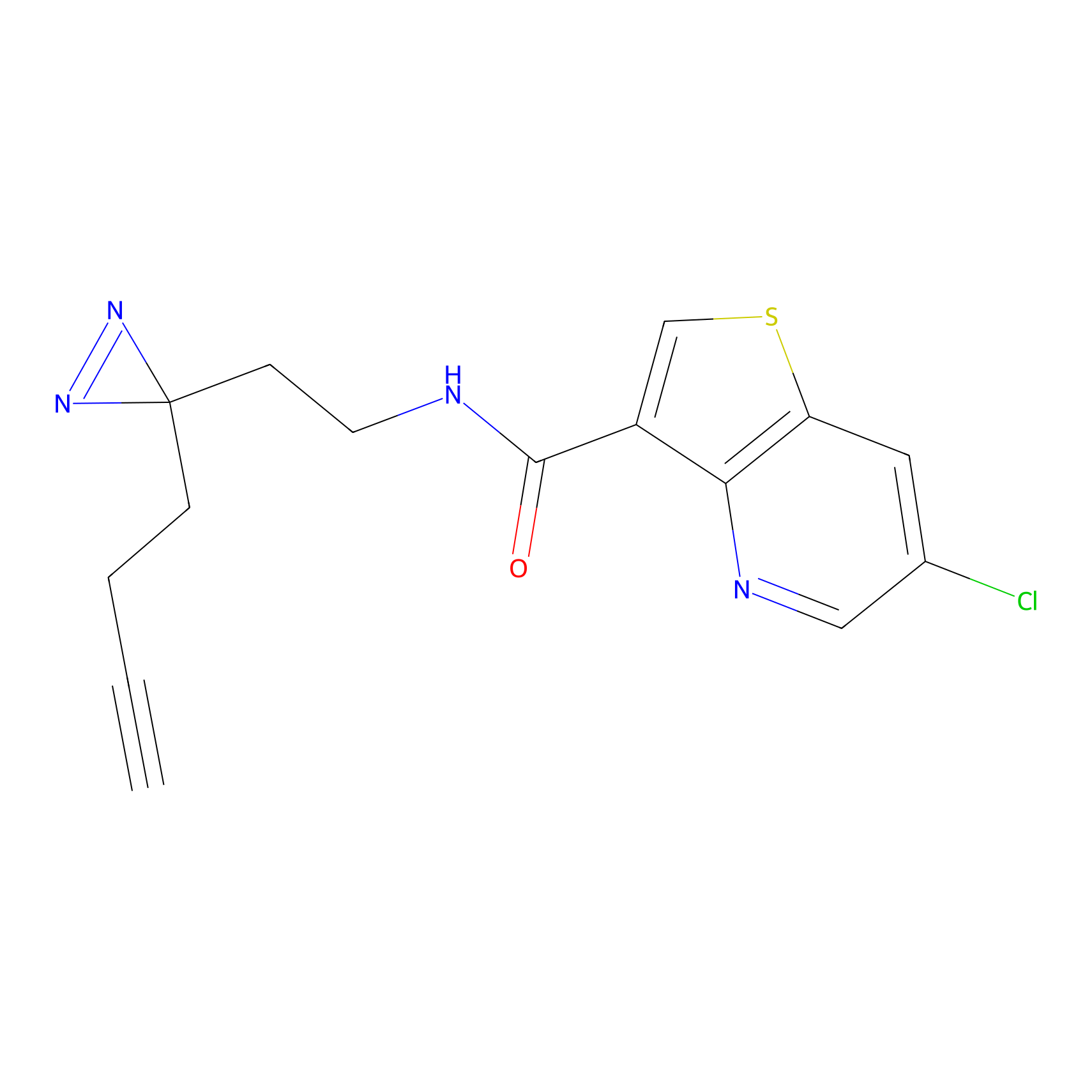
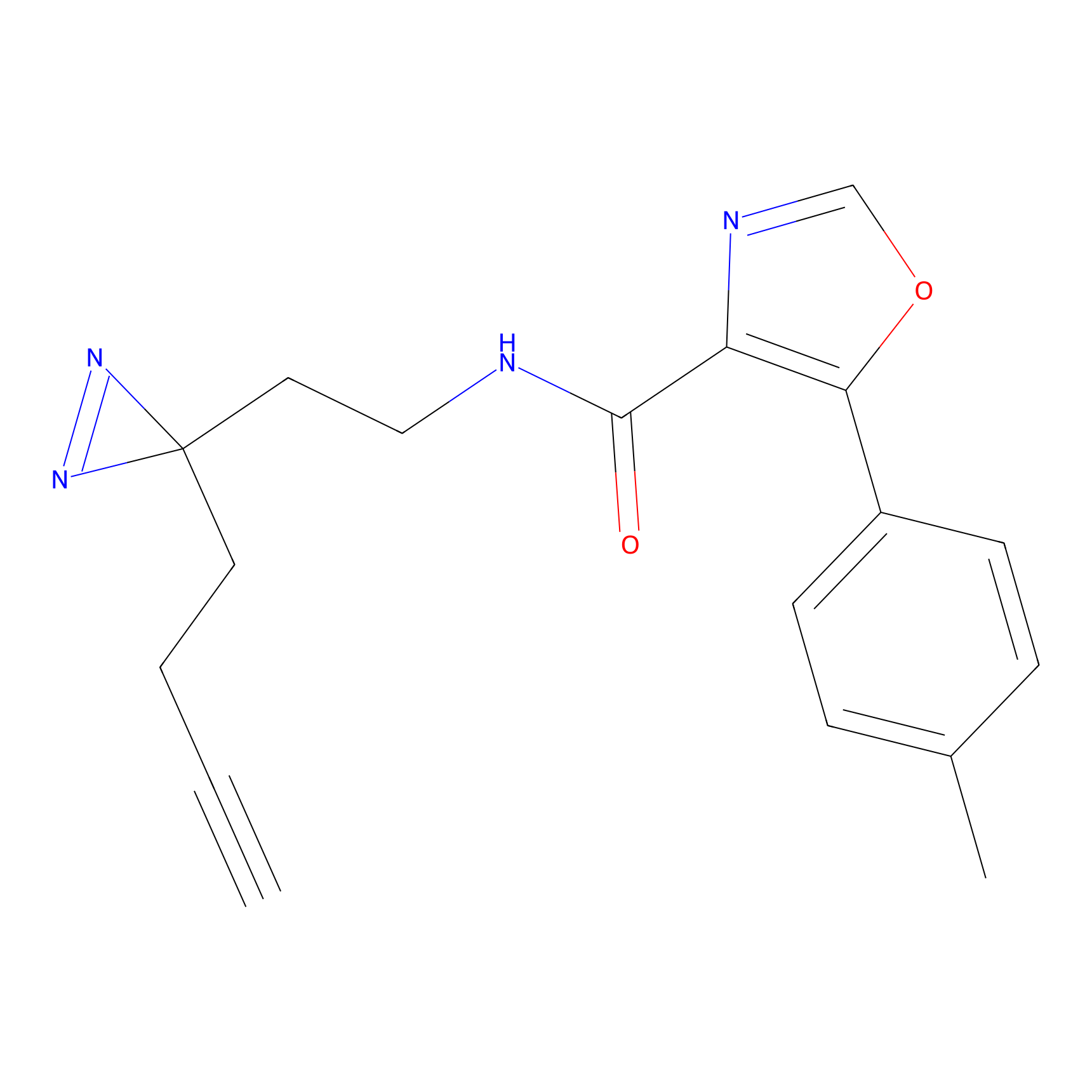
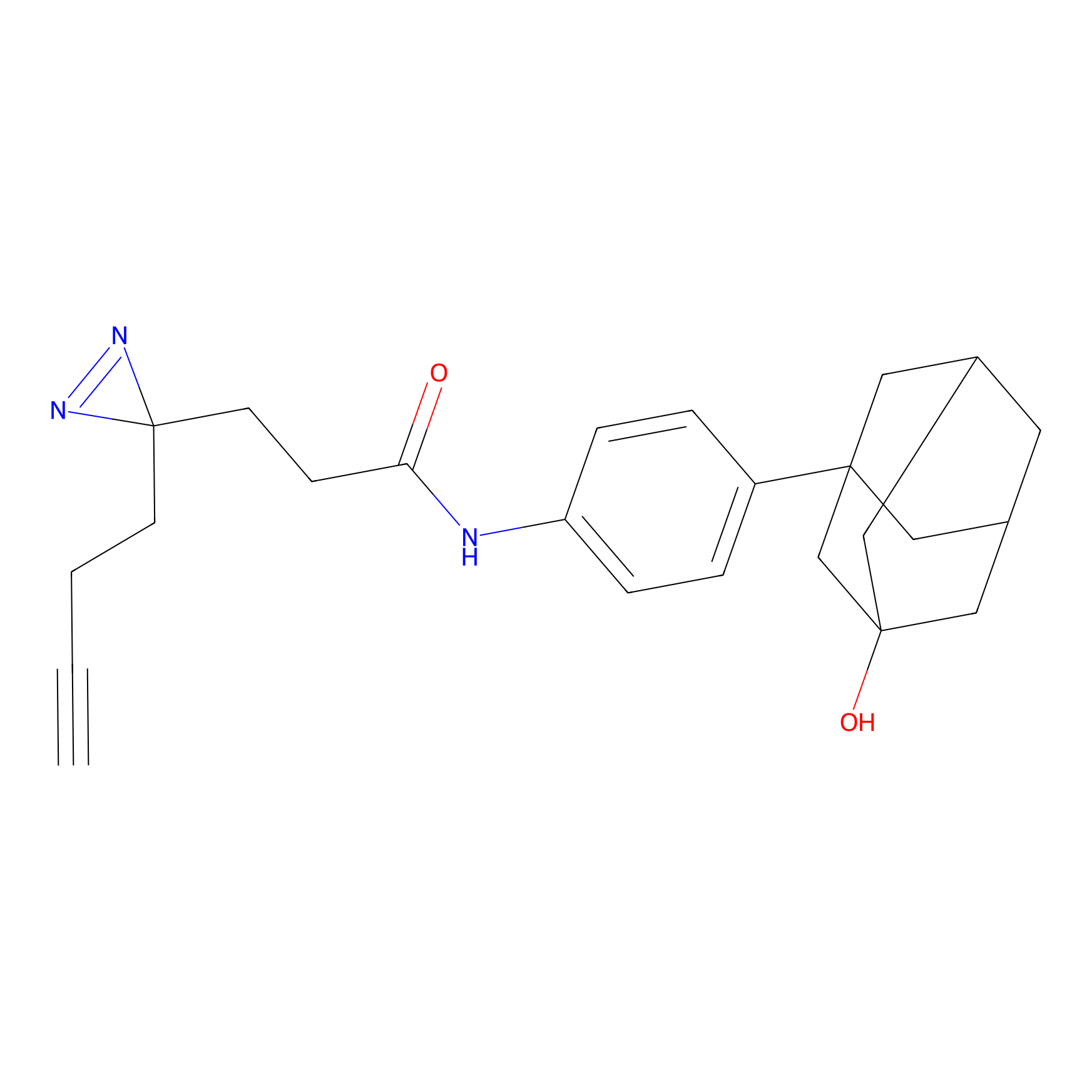
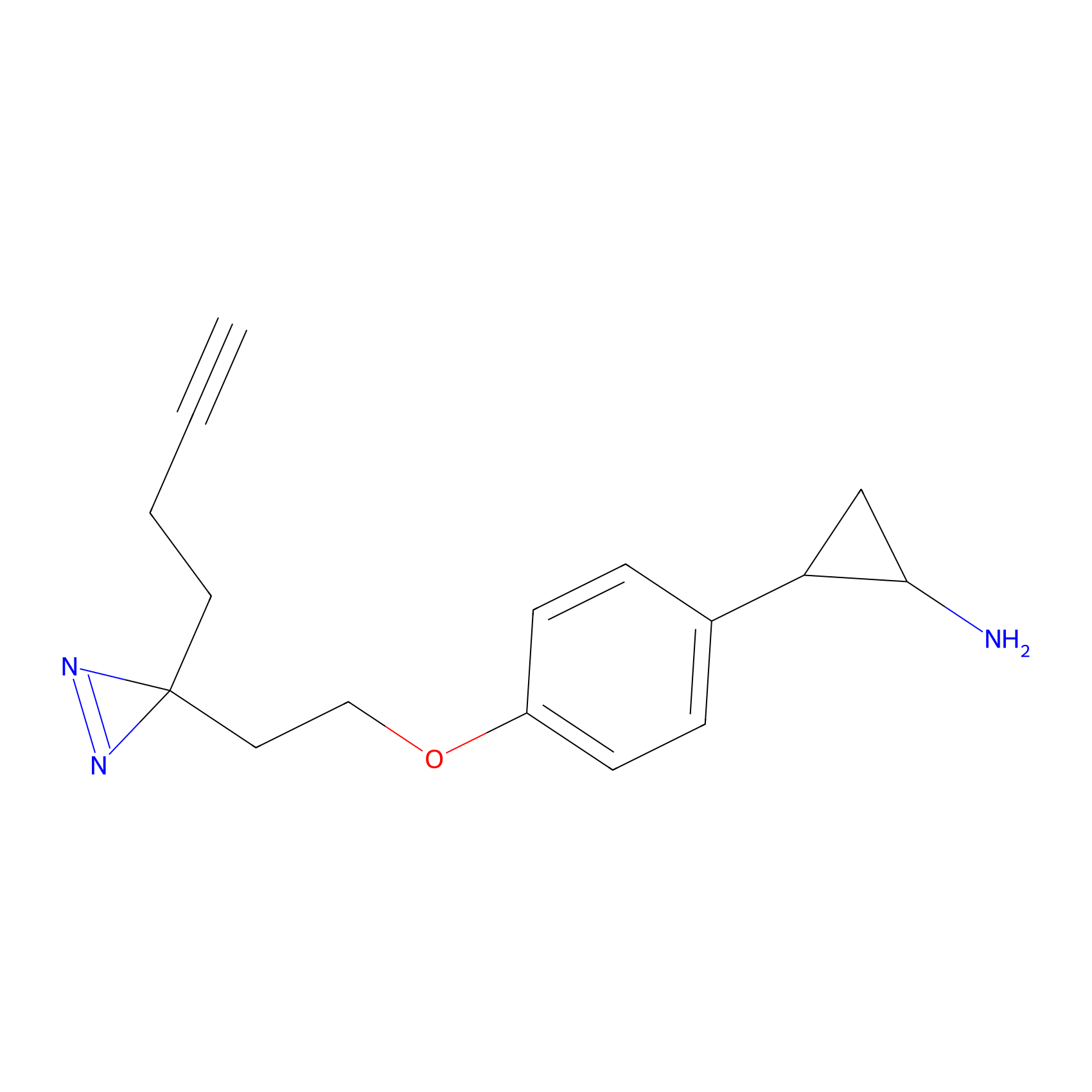
|
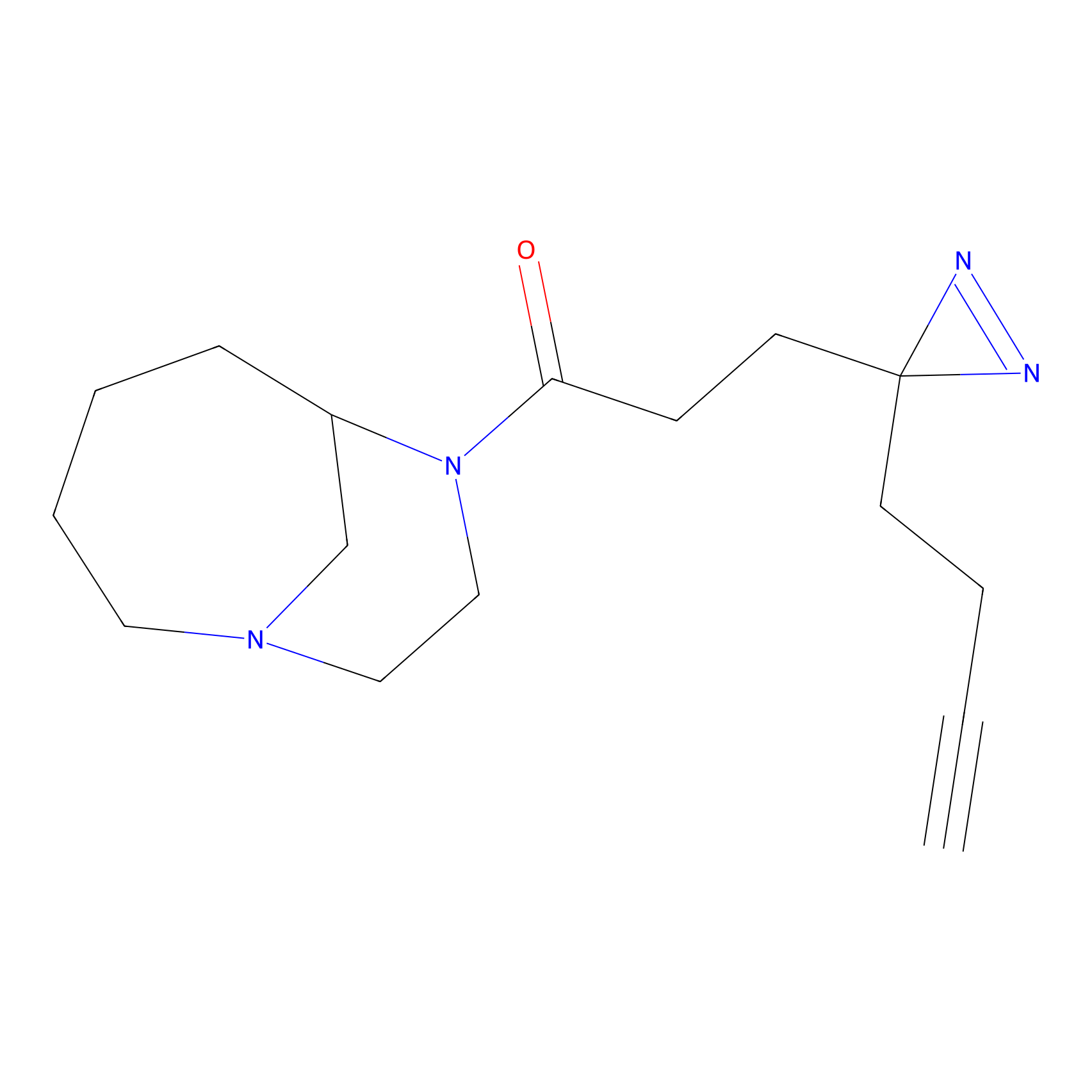
IA-alkyne Probe Info |
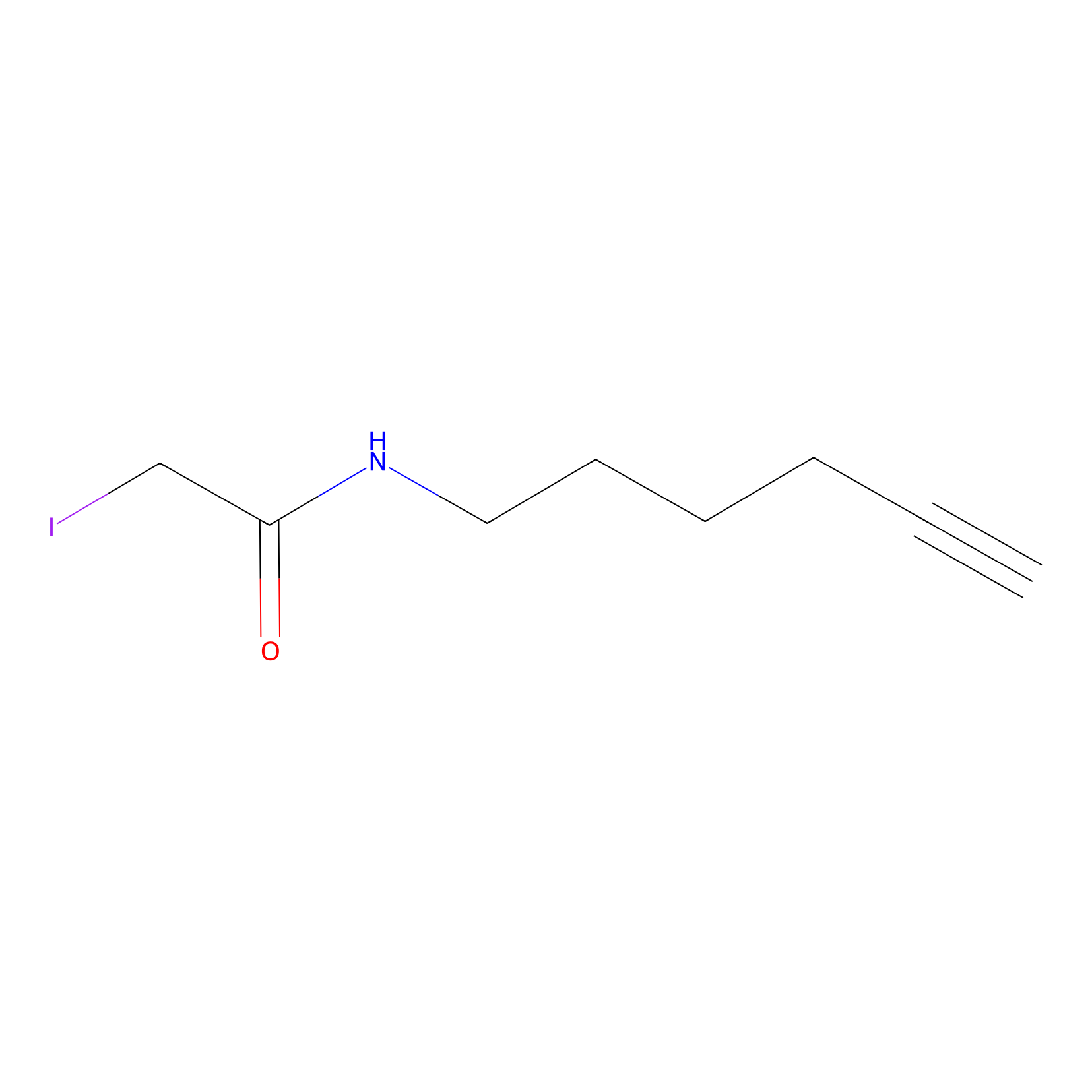 |
C237(9.84) | LDD1706 | [3] | |
|
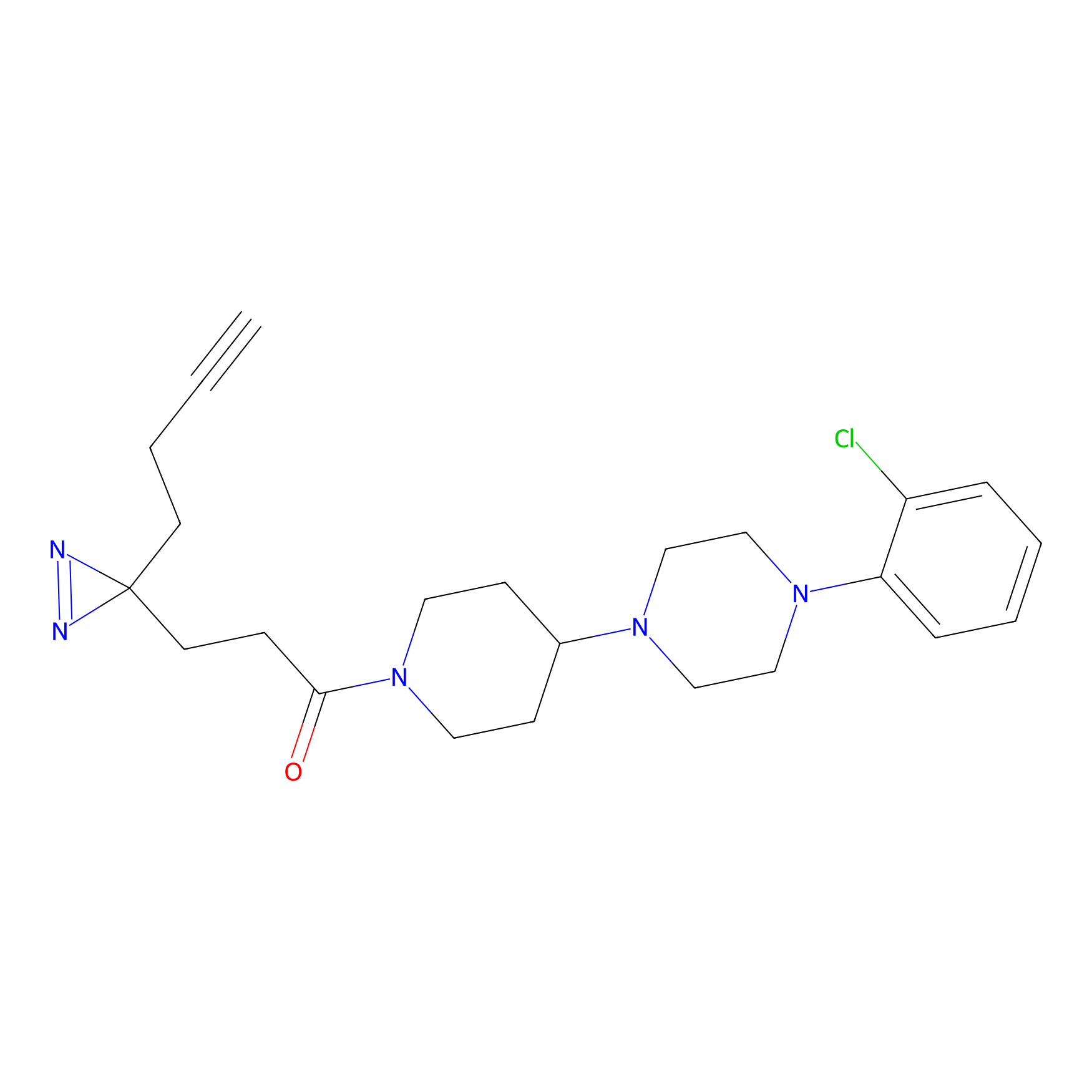
TFBX Probe Info |
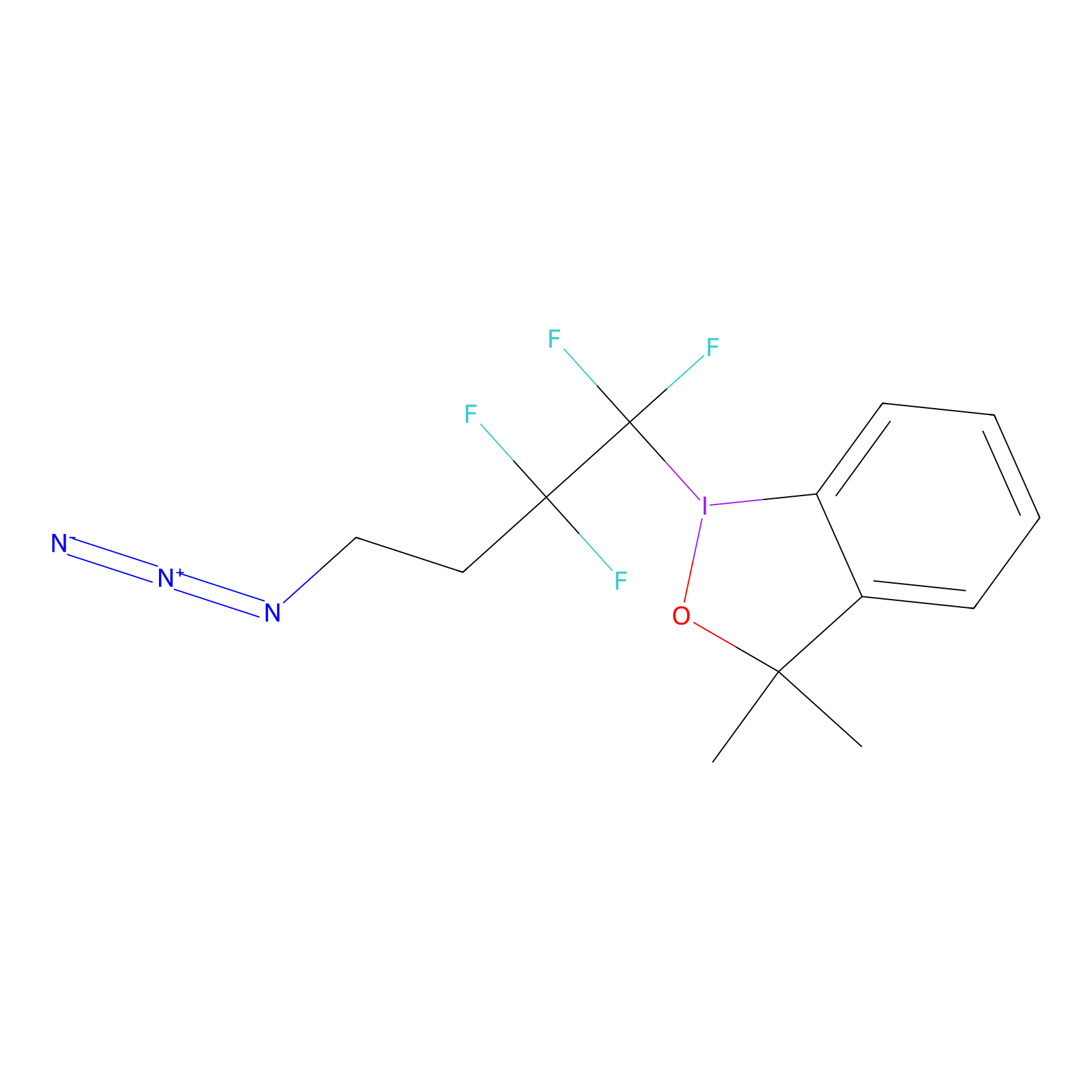 |
N.A. | LDD0148 | [4] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
References