Details of the Target
General Information of Target
| Target ID | LDTP18153 | |||||
|---|---|---|---|---|---|---|
| Target Name | Major facilitator superfamily domain-containing protein 3 (MFSD3) | |||||
| Gene Name | MFSD3 | |||||
| Gene ID | 113655 | |||||
| Synonyms |
Major facilitator superfamily domain-containing protein 3 |
|||||
| 3D Structure | ||||||
| Sequence |
MDRNPSPPPPGRDKEEEEEVAGGDCIGSTVYSKHWLFGVLSGLIQIVSPENTKSSSDDEE
QLTELDEEMENEICRVWDMSMDEDVALFLQEFNAPDIFMGVLAKSKCPRLREICVGILGN MACFQEICVSISSDKNLGQVLLHCLYDSDPPTLLETSRLLLTCLSQAEVASVWVERIQEH PAIYDSICFIMSSSTNVDLLVKVGEVVDKLFDLDEKLMLEWVRNGAAQPLDQPQEESEEQ PVFRLVPCILEAAKQVRSENPEWLDVYMHILQLLTTVDDGIQAIVHCPDTGKDIWNLLFD LVCHEFCQSDDPPIILQEQKTVLASVFSVLSAIYASQTEQEYLKIEKVDLPLIDSLIRVL QNMEQCQKKPENSAESNTEETKRTDLTQDDFHLKILKDILCEFLSNIFQALTKETVAQGV KEGQLSKQKCSSAFQNLLPFYSPVVEDFIKILREVDKALADDLEKNFPSLKVQT |
|||||
| Target Bioclass |
Transporter and channel
|
|||||
| Family |
Major facilitator superfamily
|
|||||
| Subcellular location |
Membrane
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Probe(s) Labeling This Target
ABPP Probe
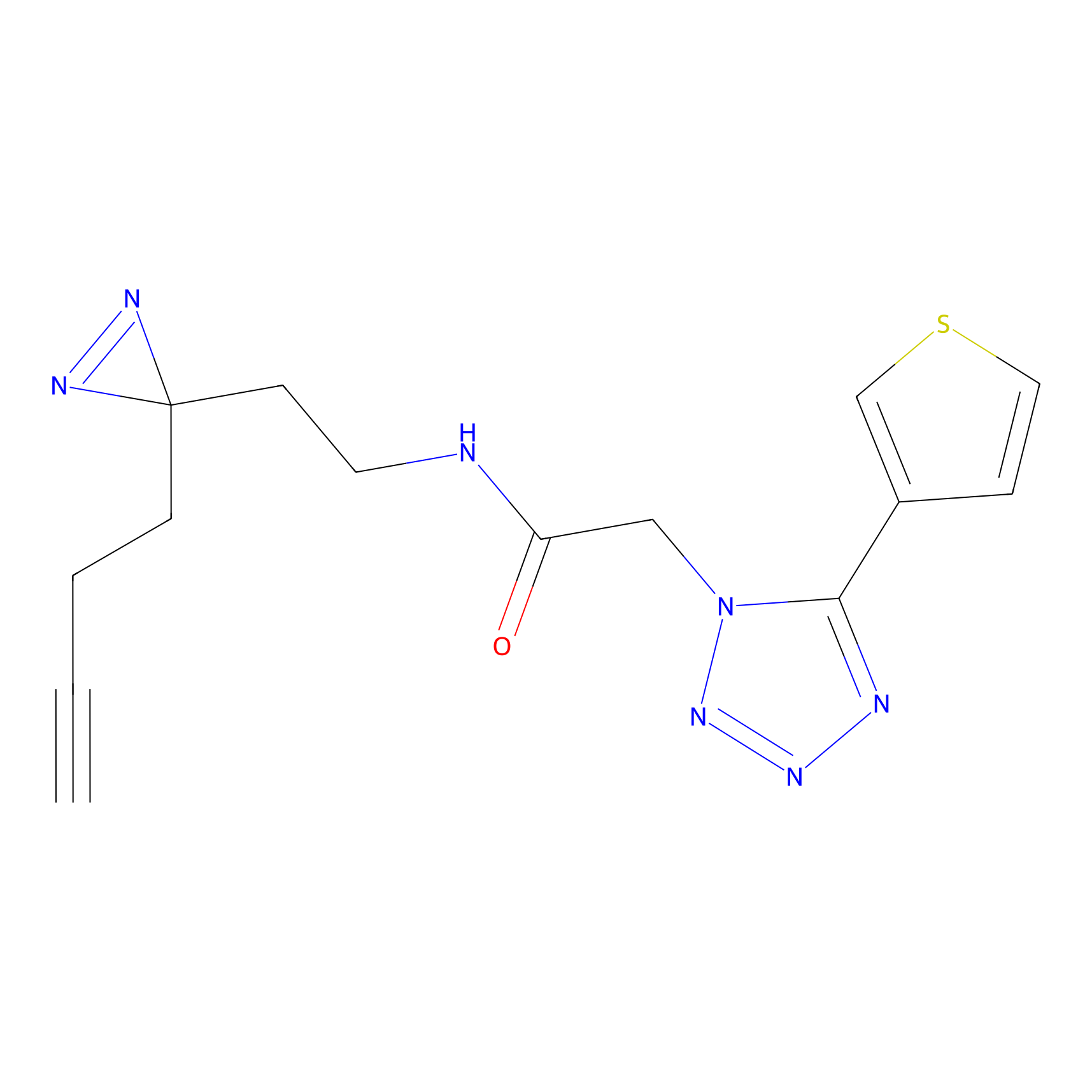
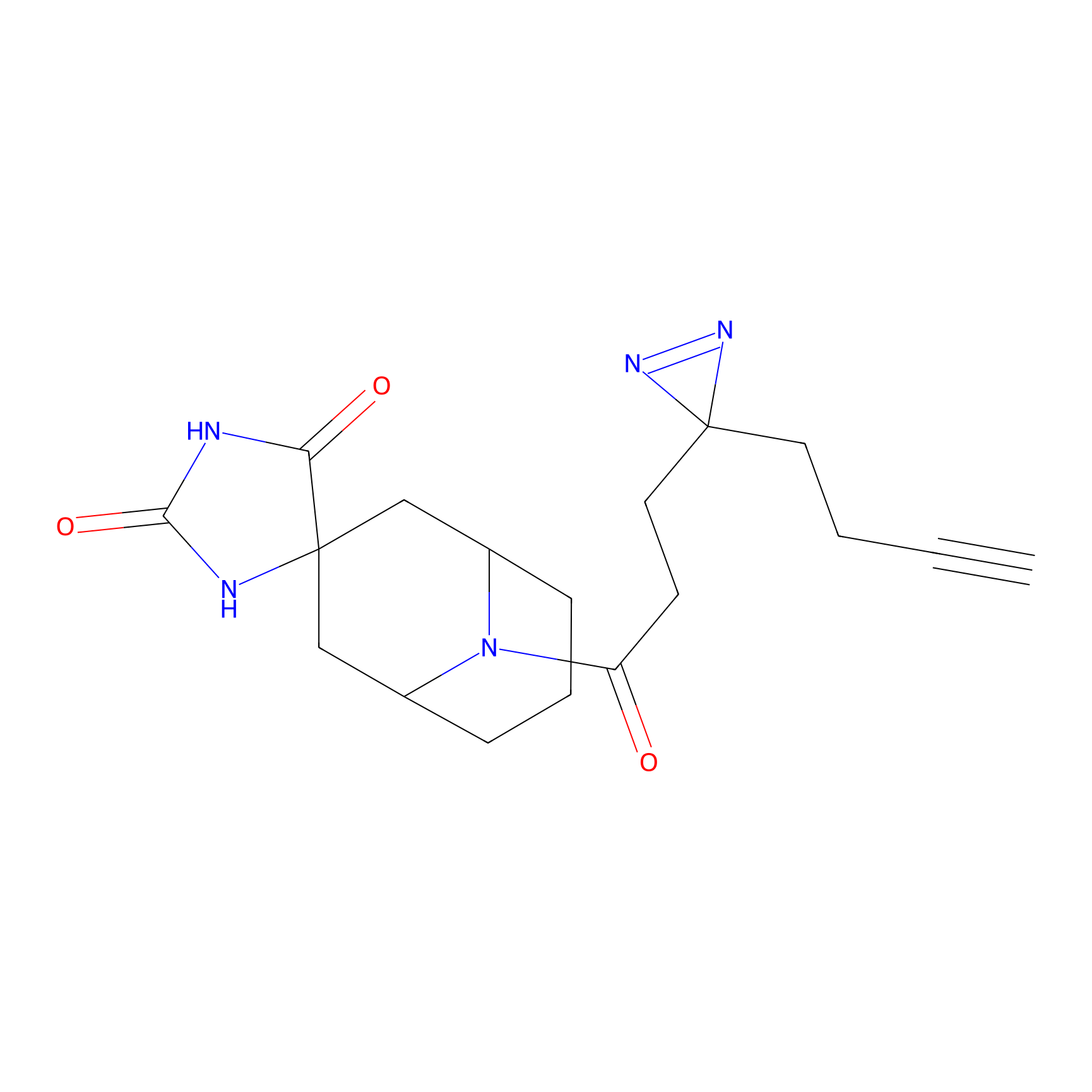
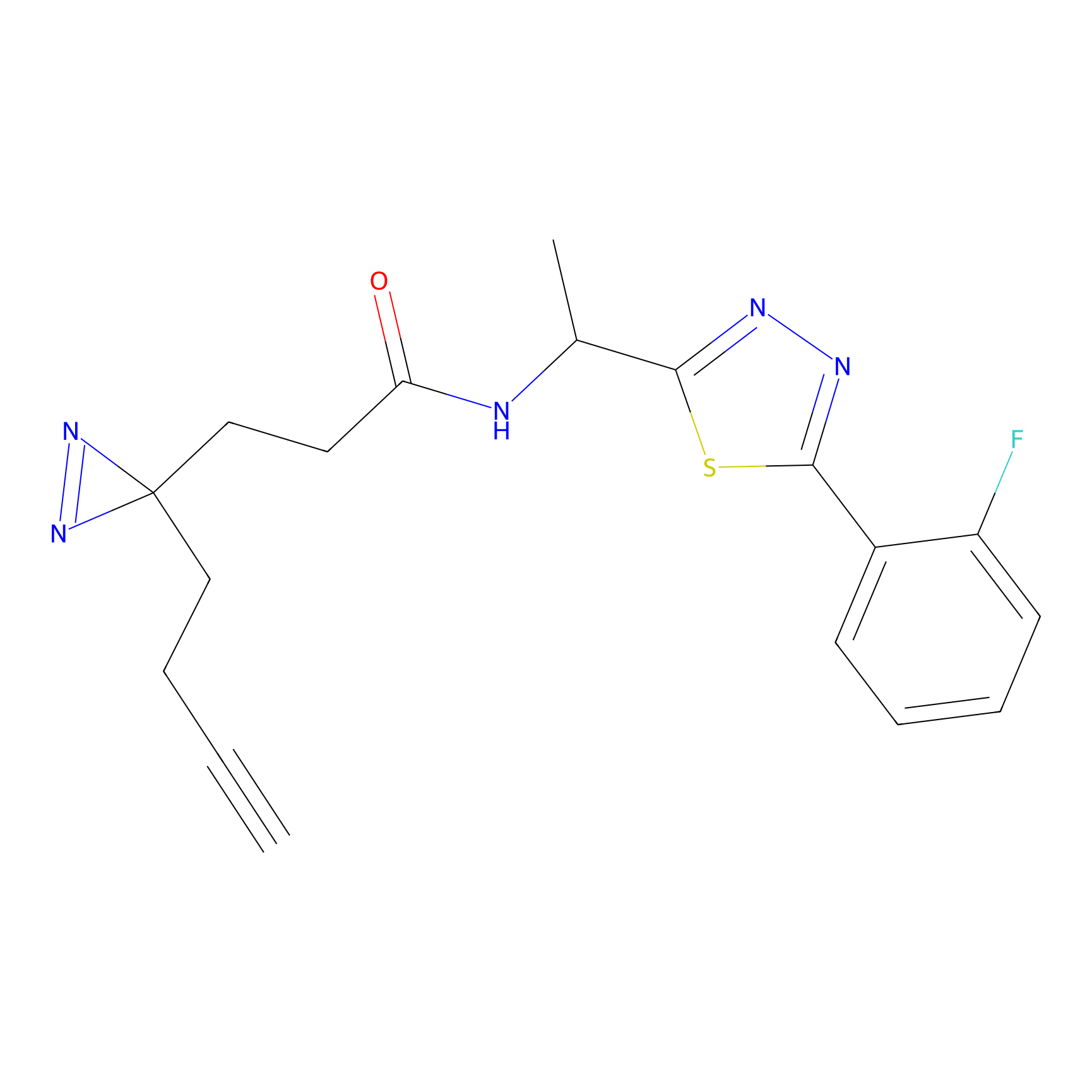
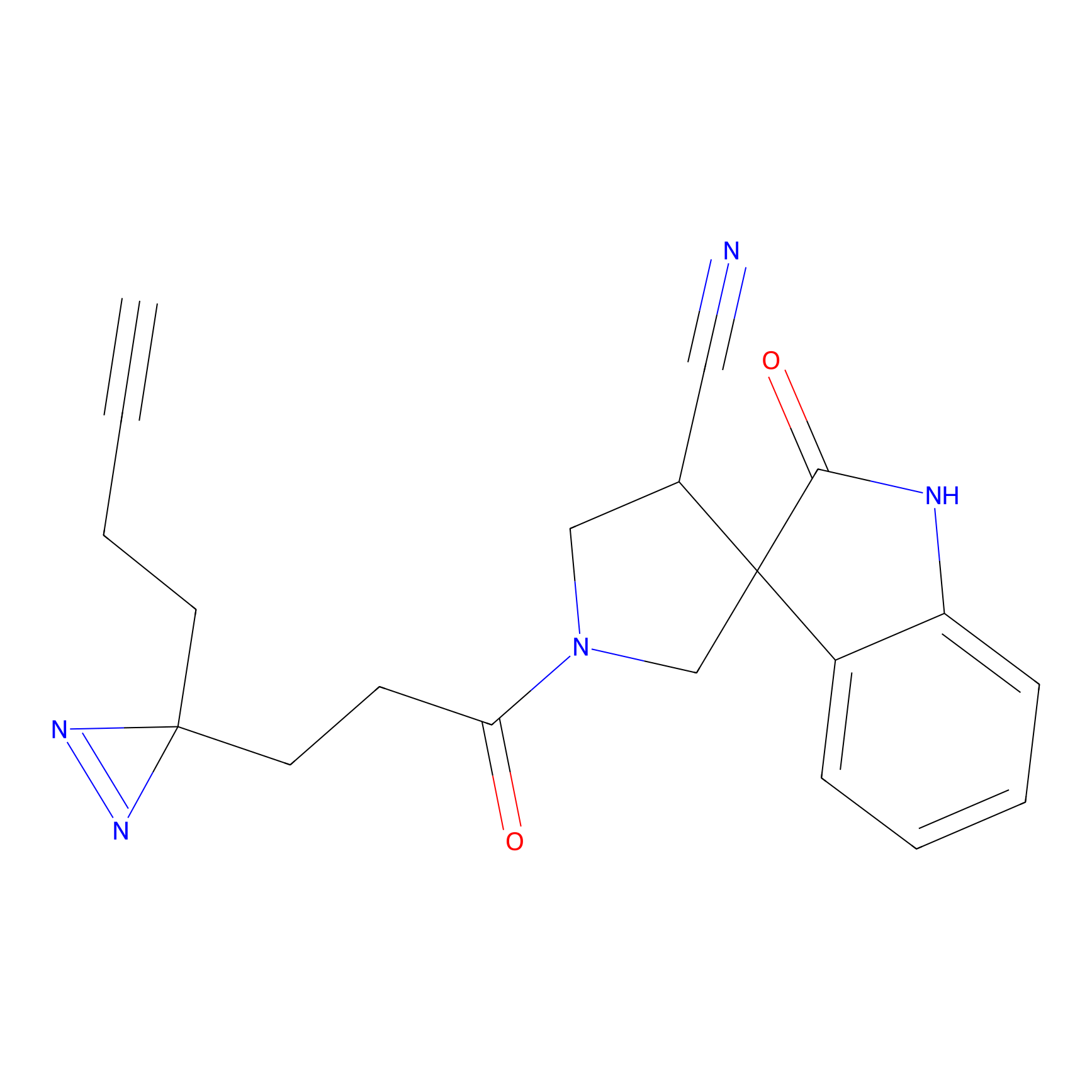
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
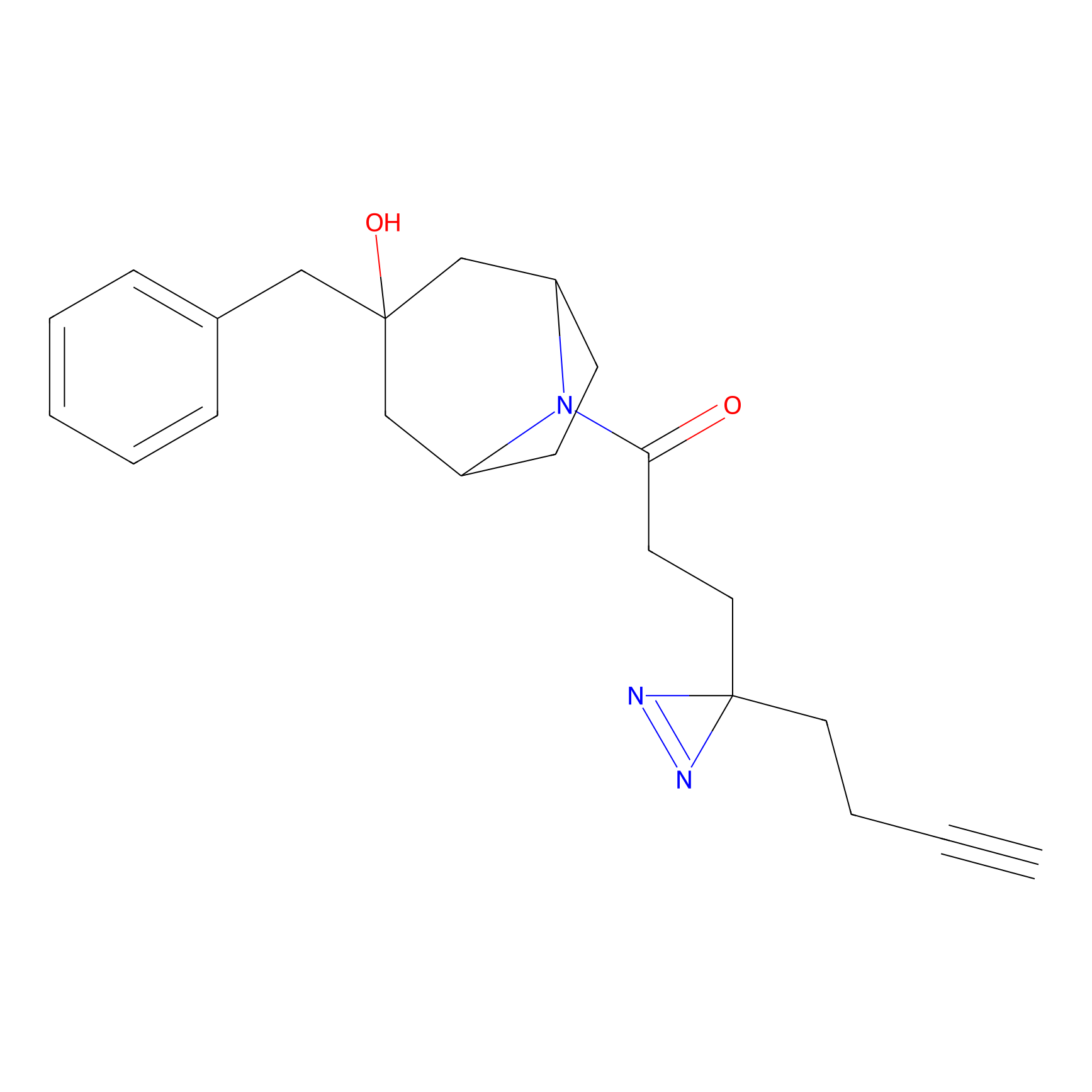
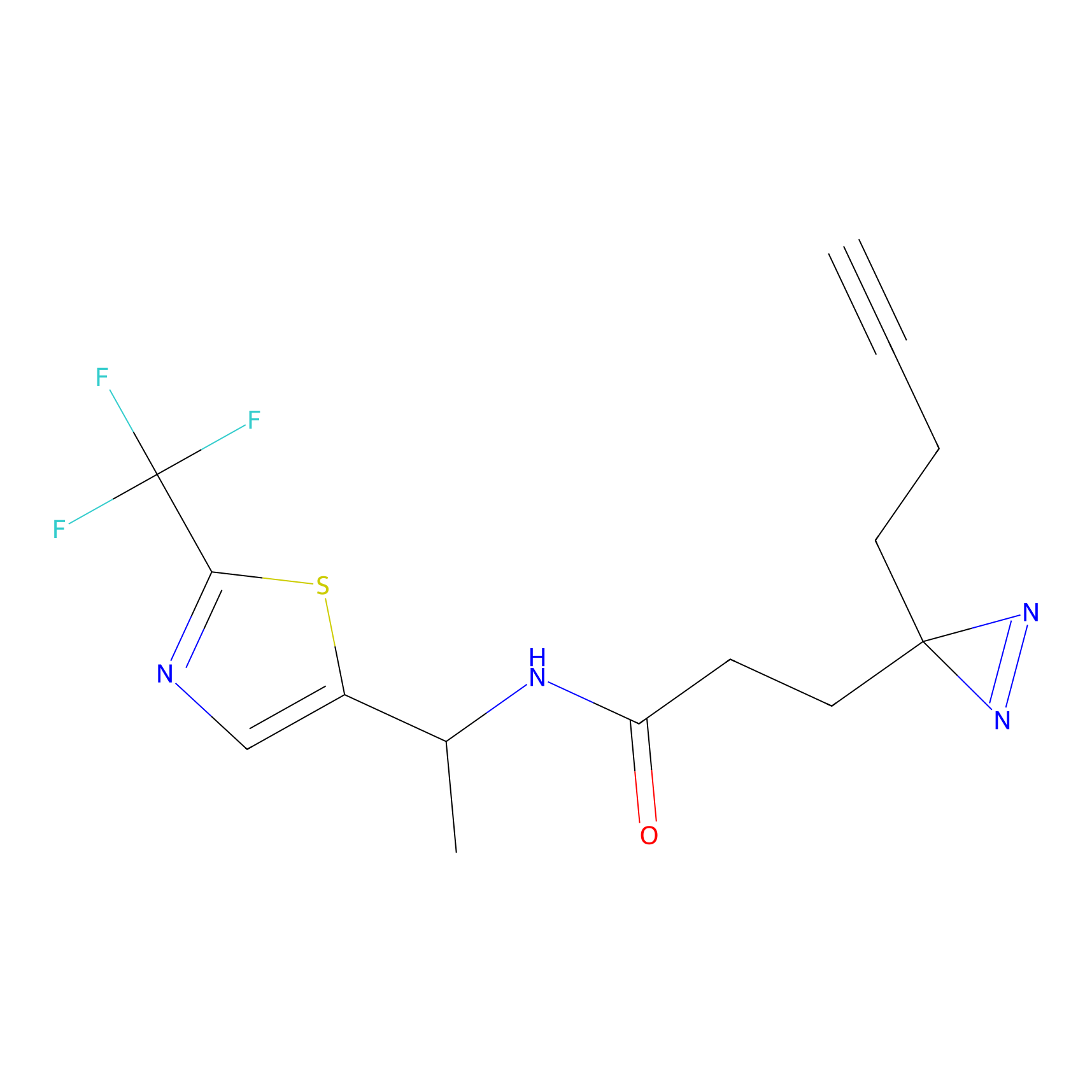
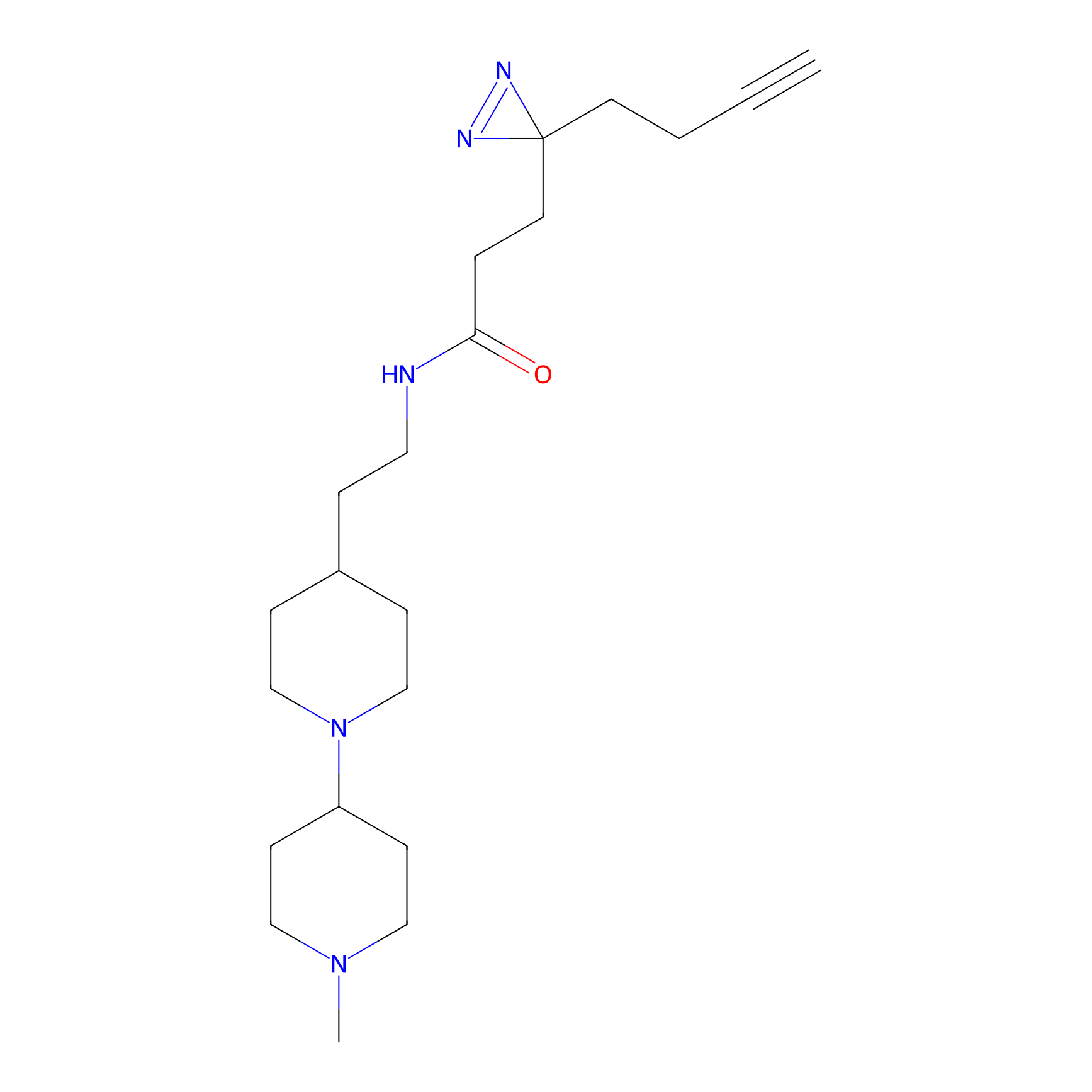
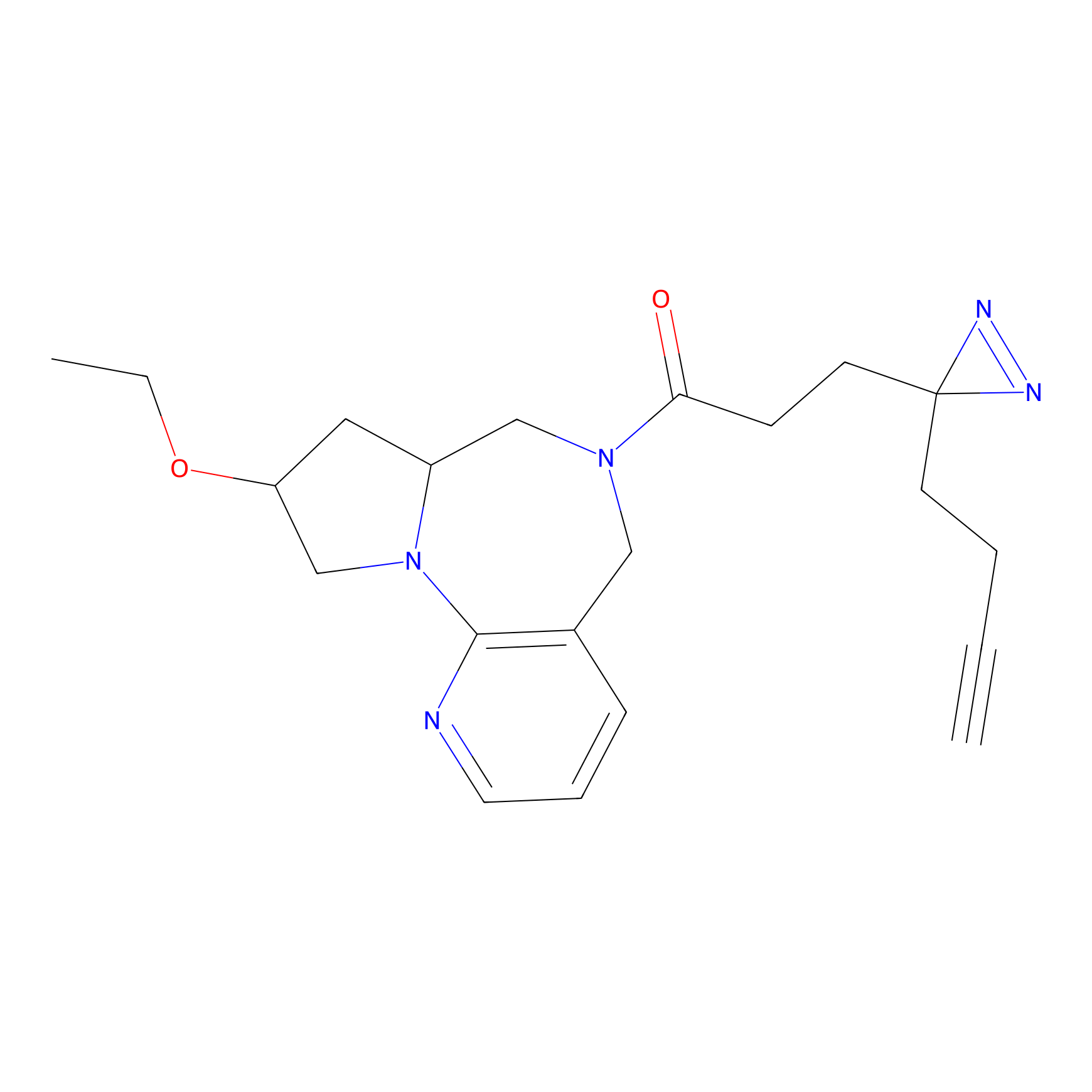
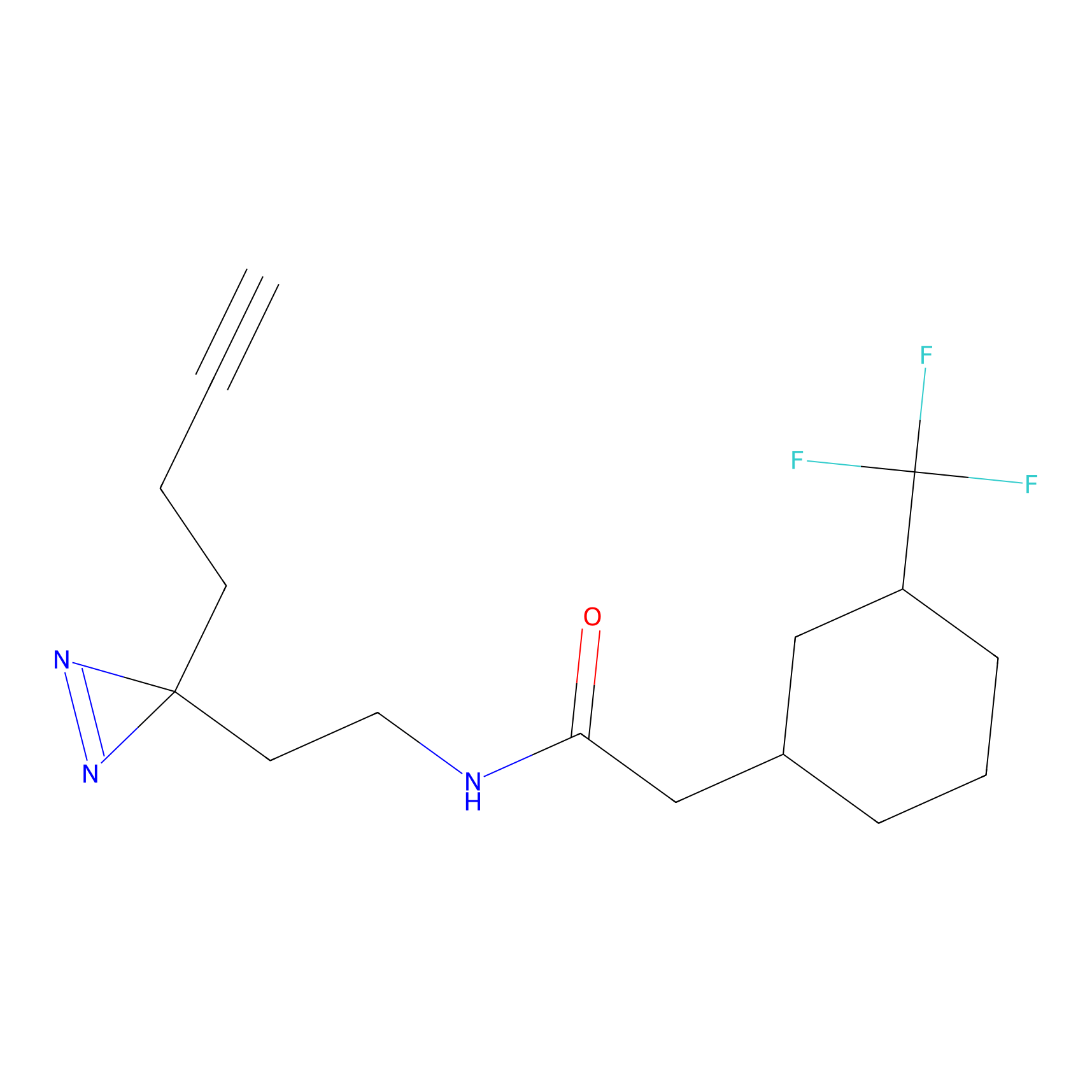
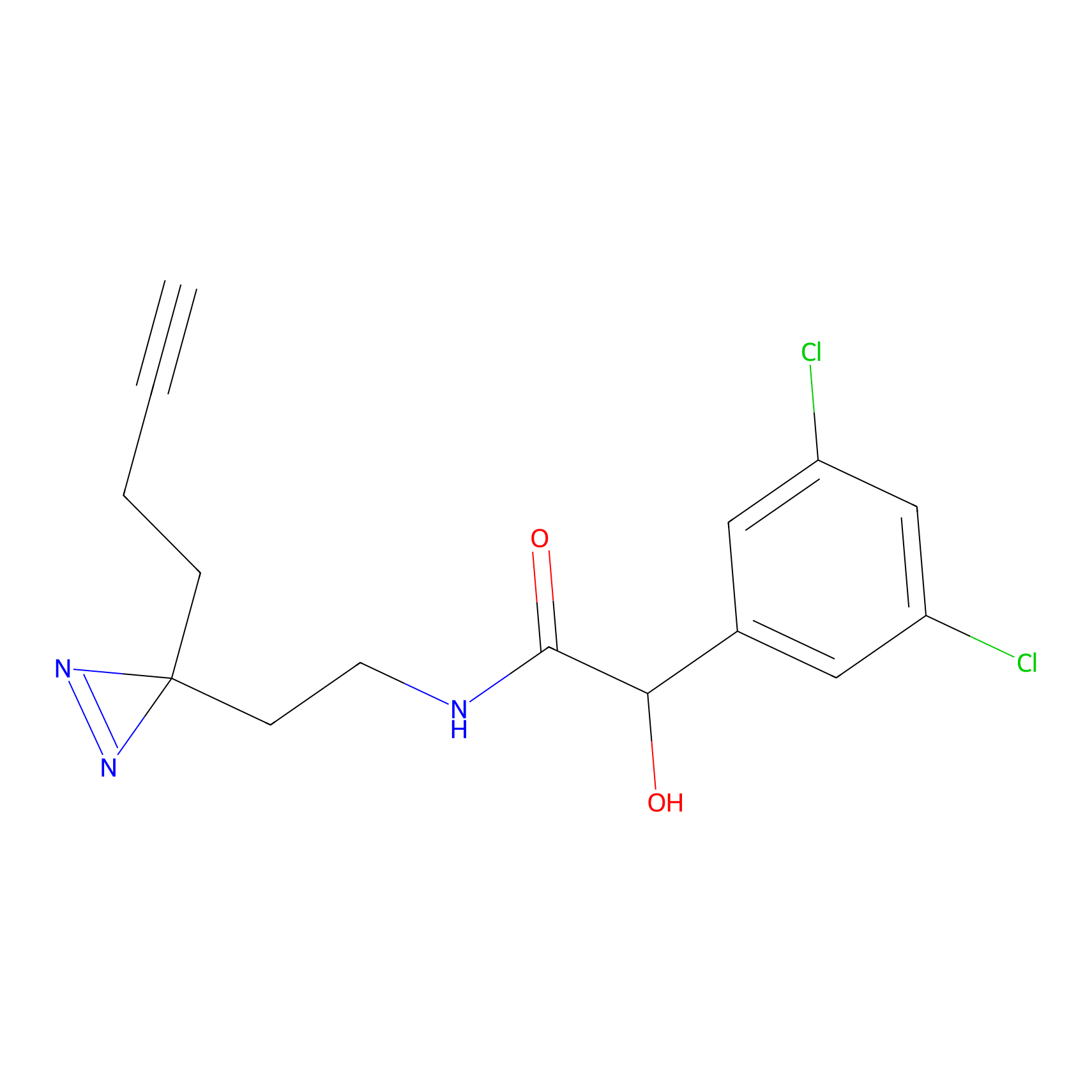
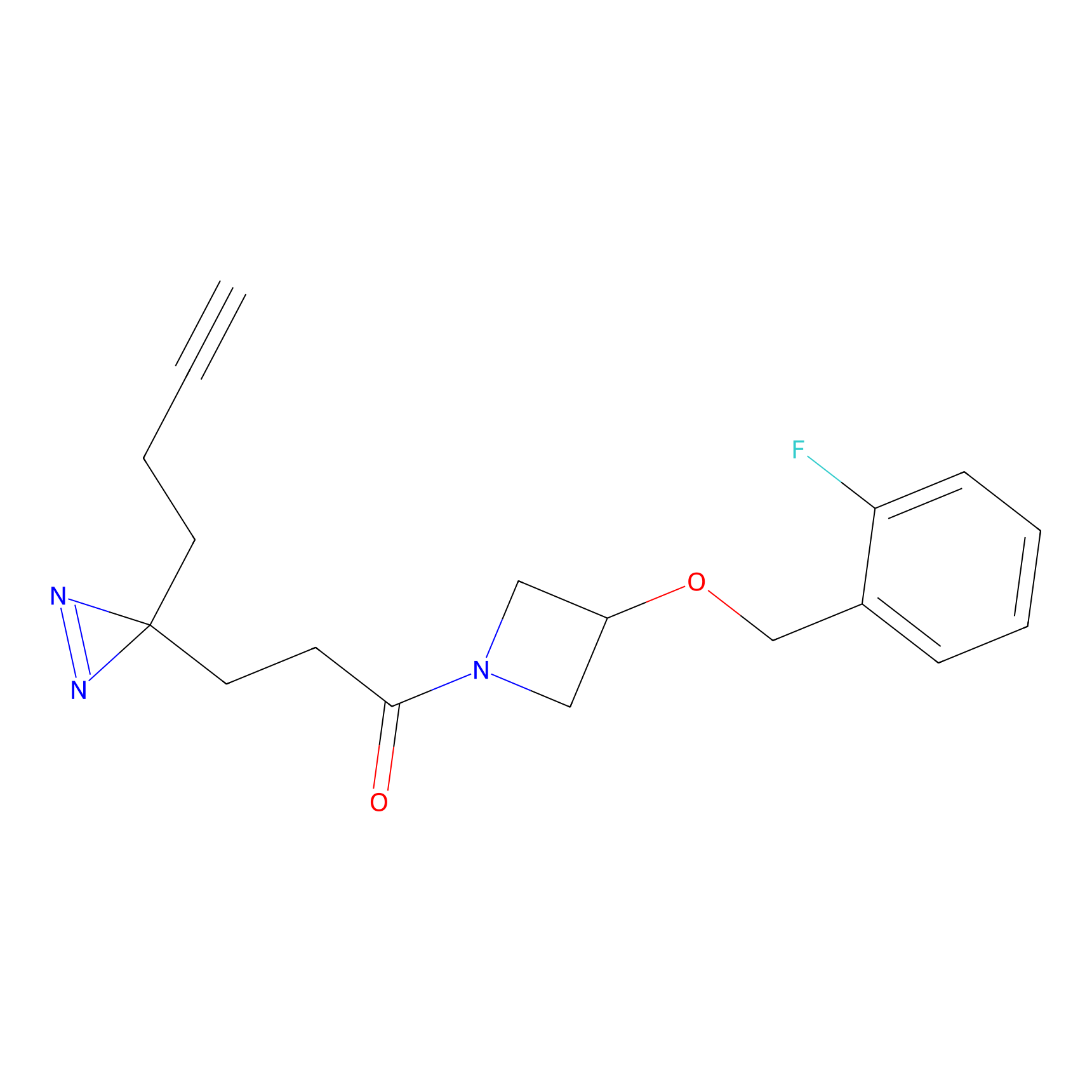
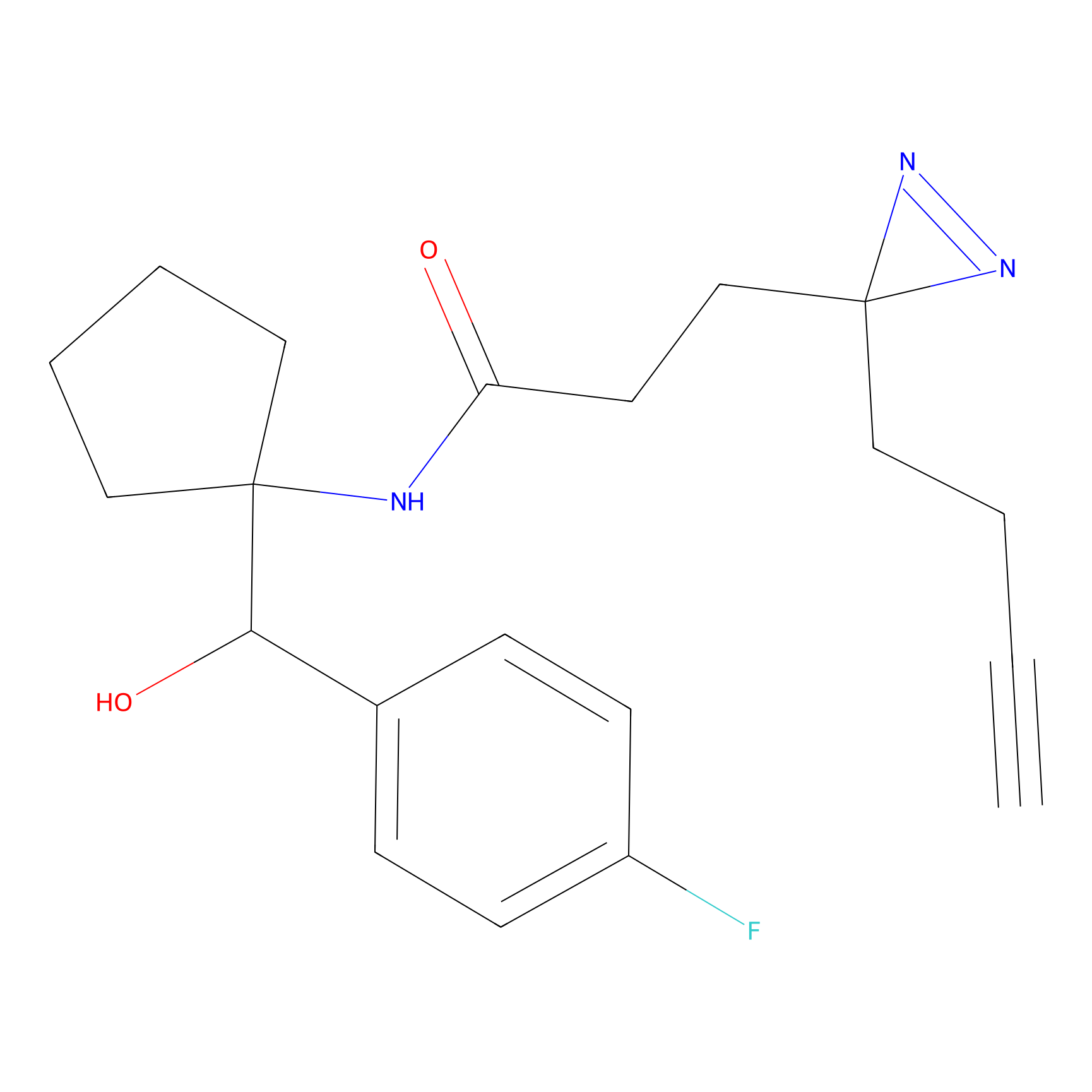
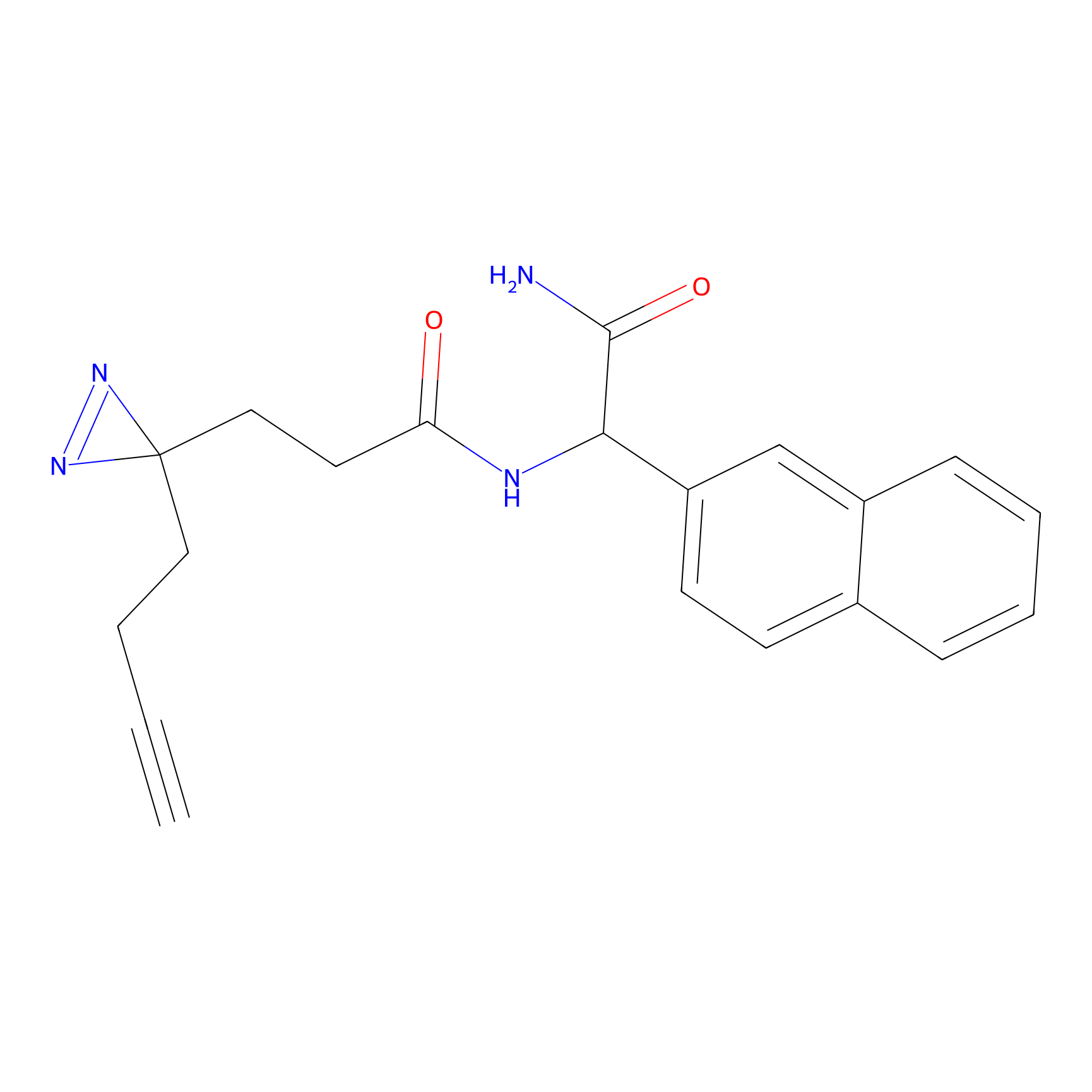
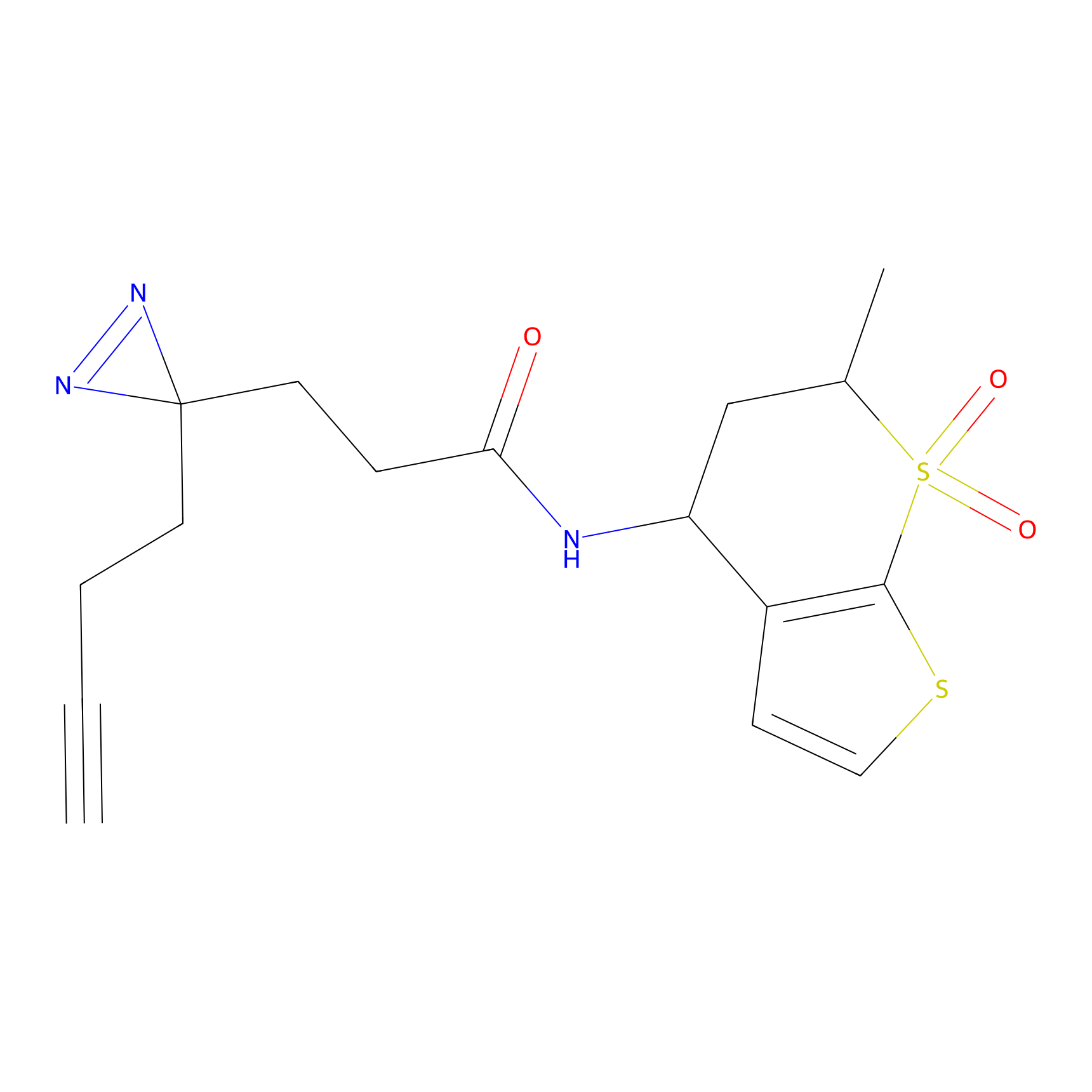
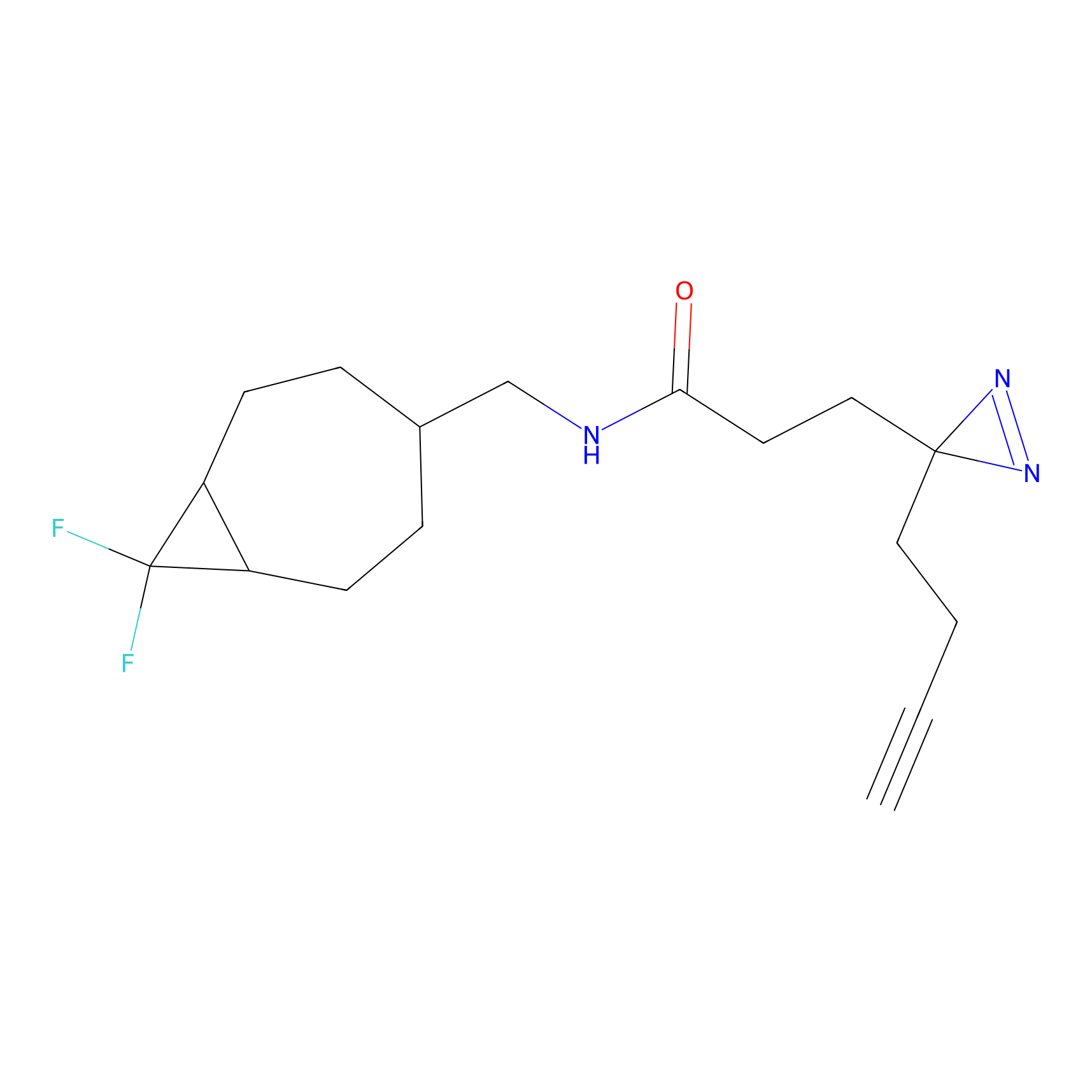
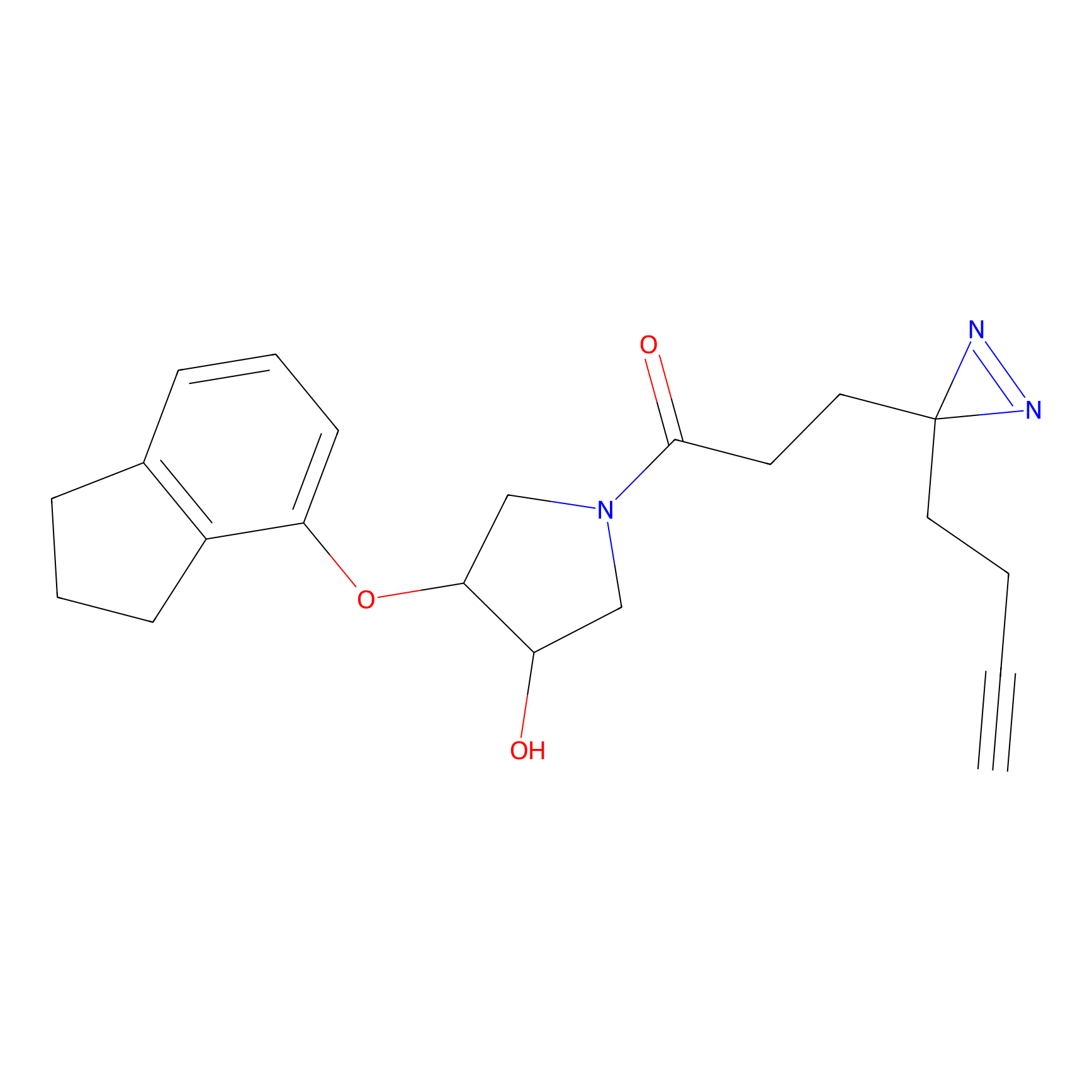
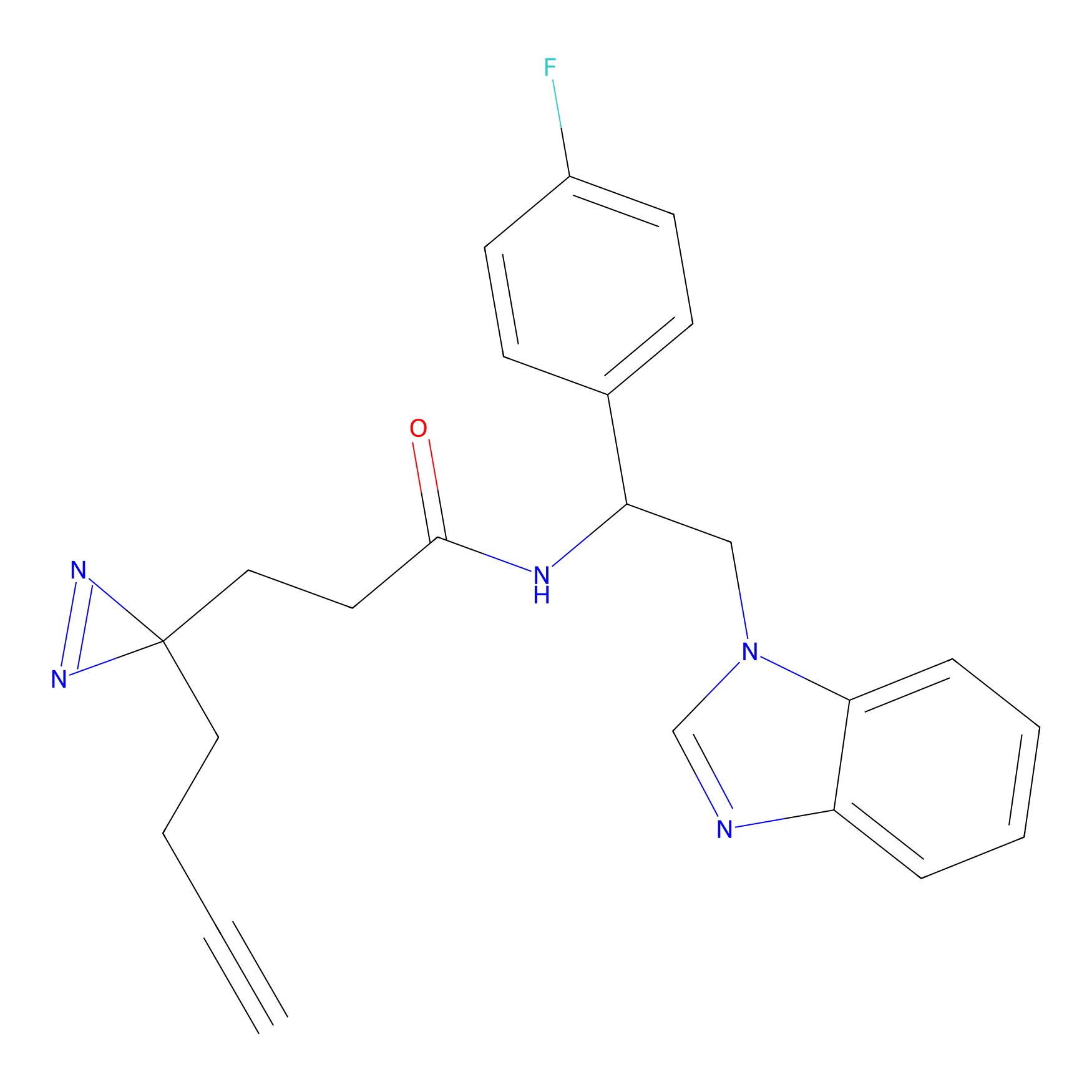
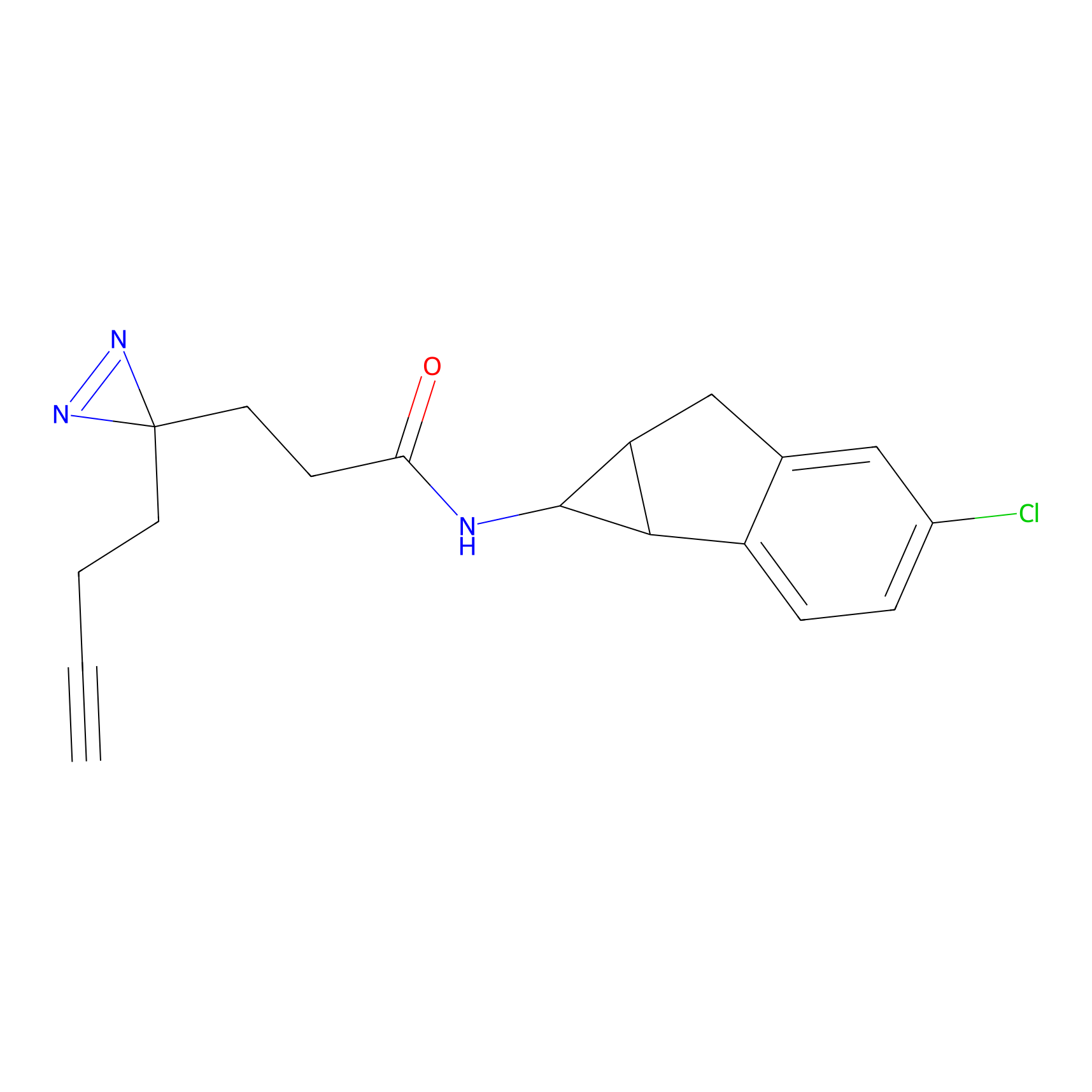
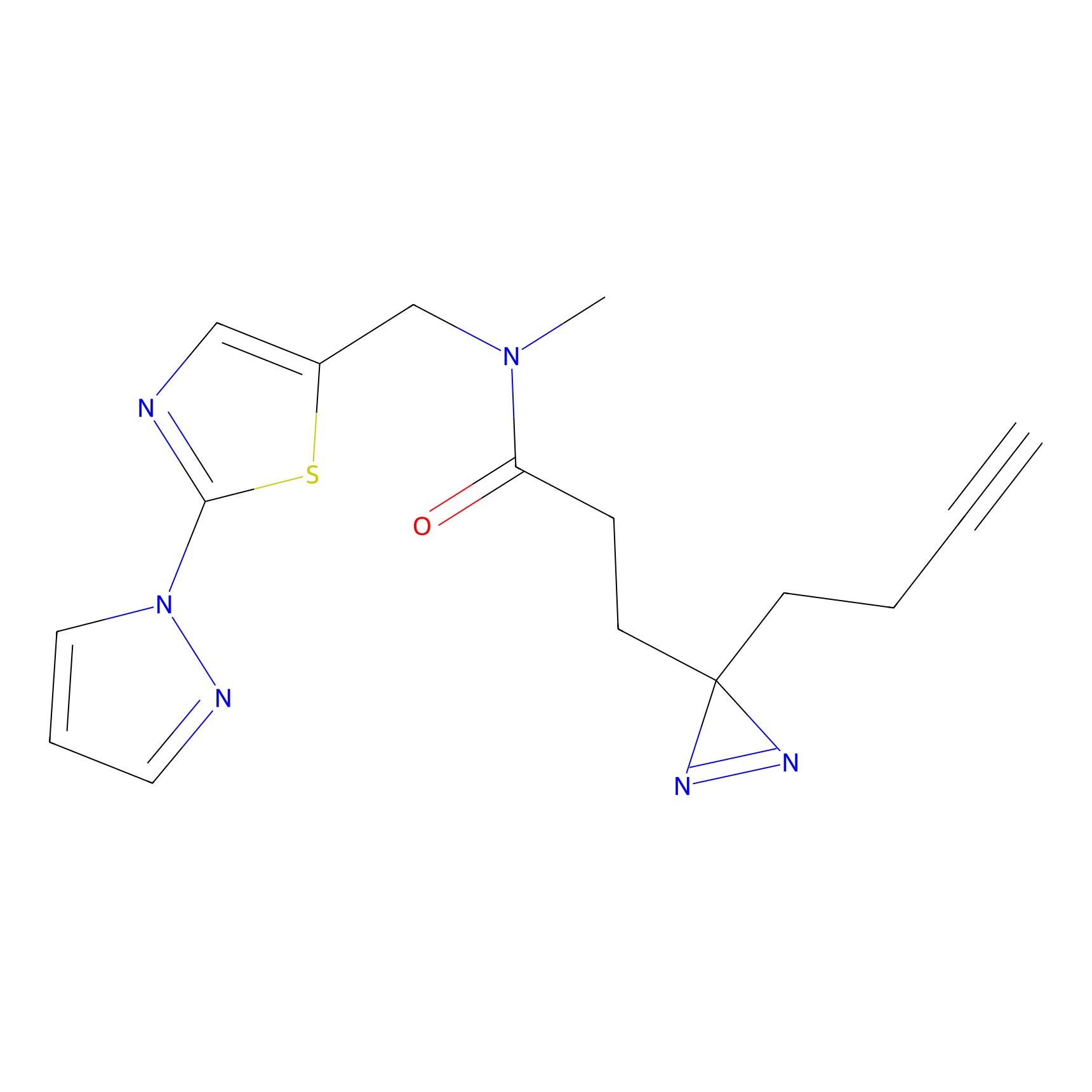
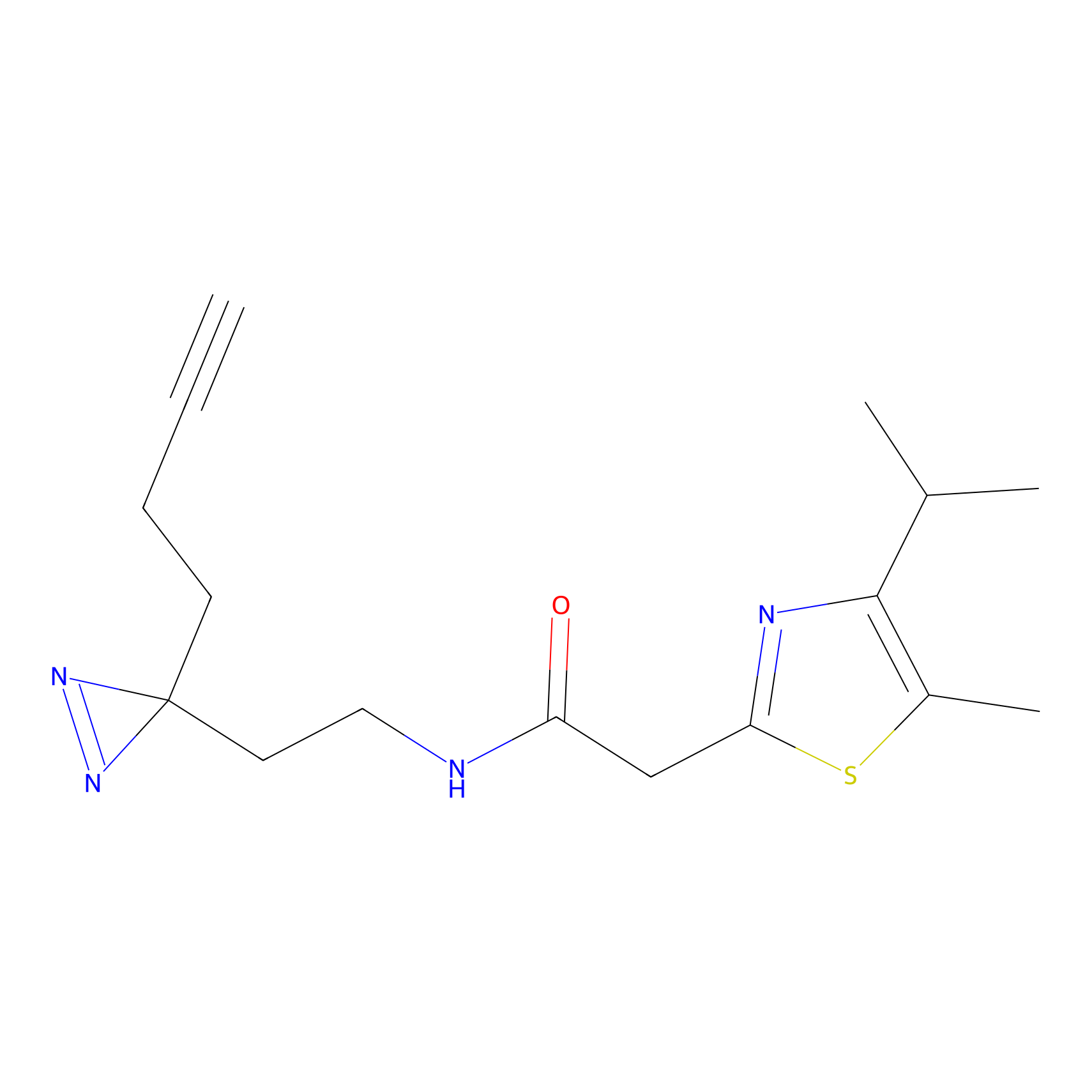
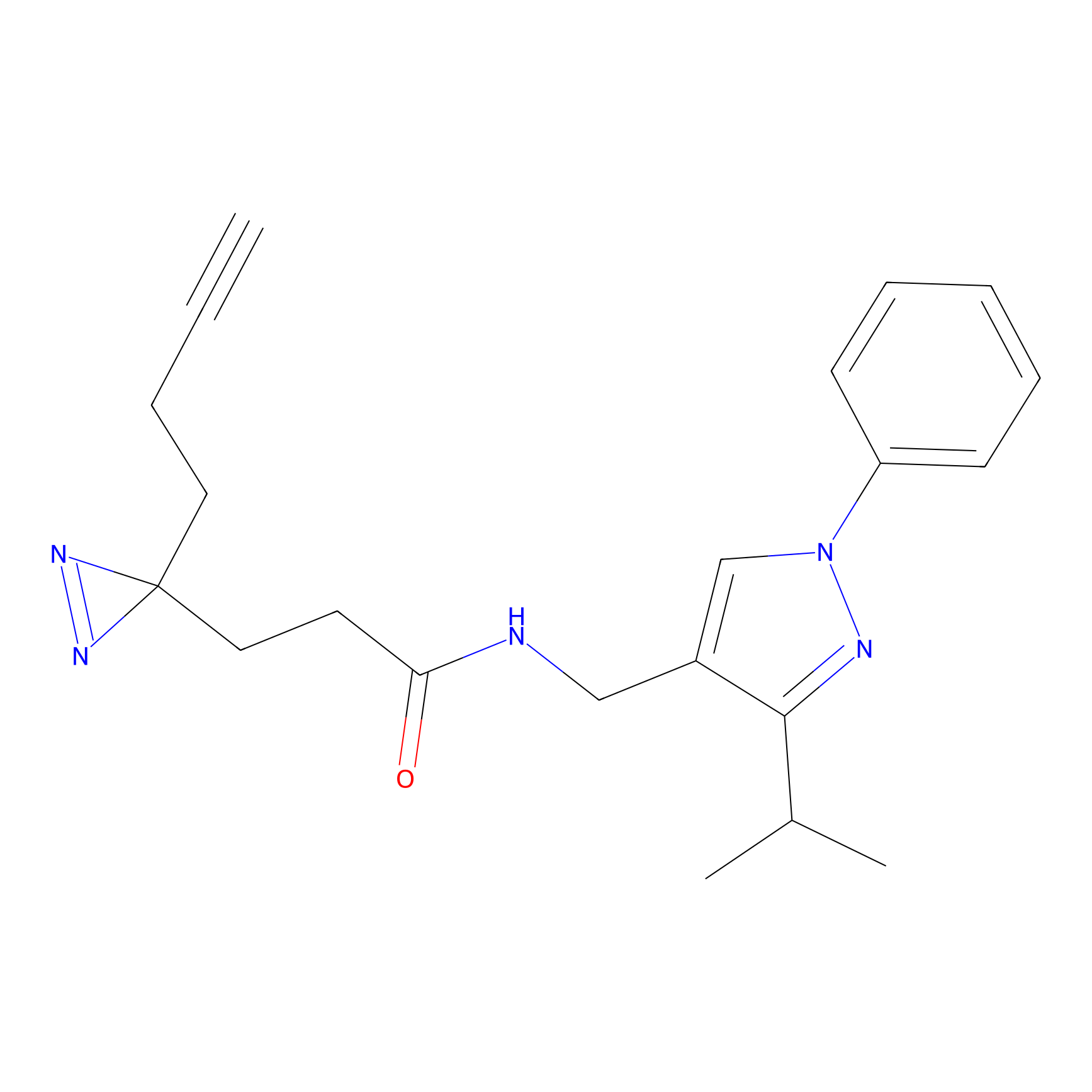
|
IA-alkyne Probe Info |
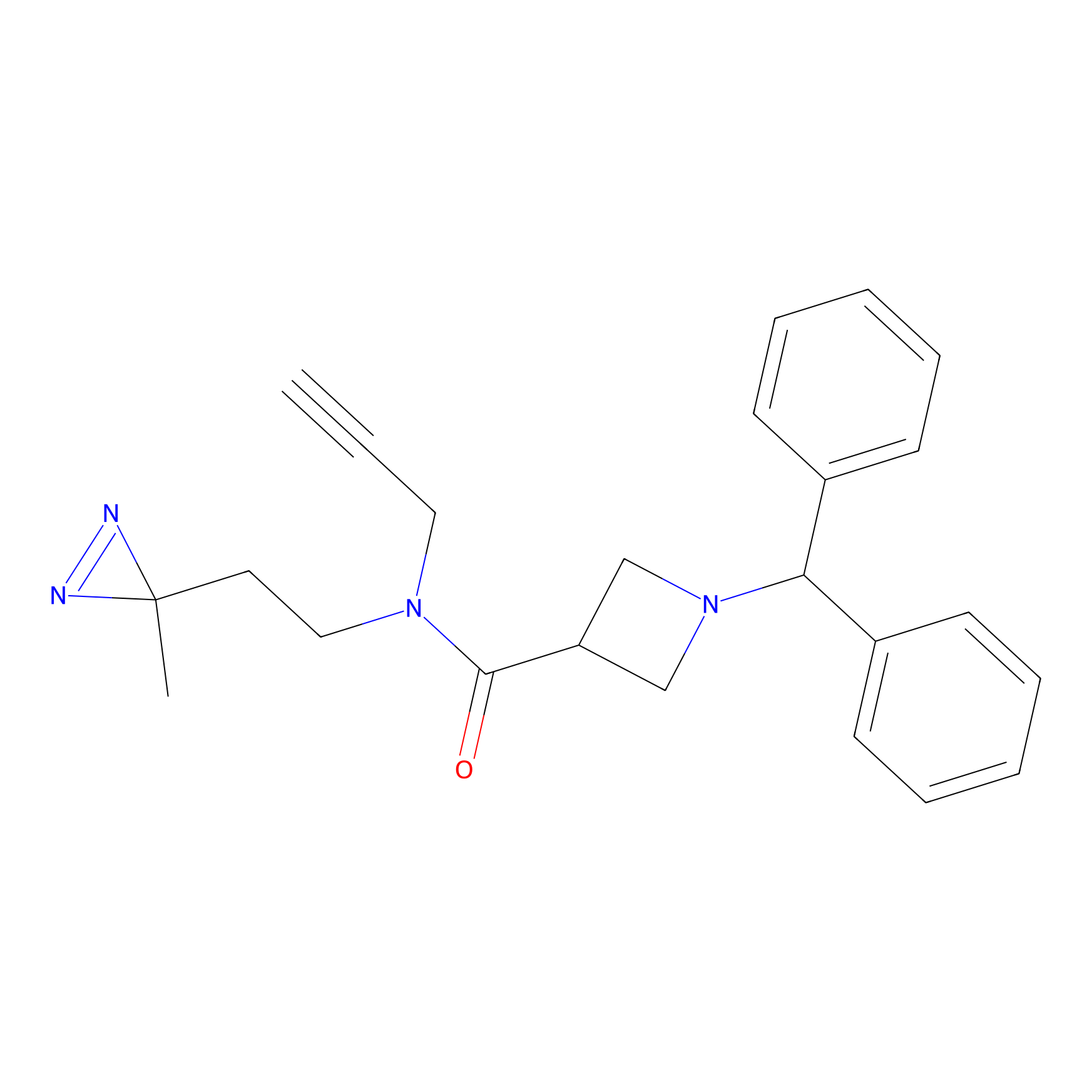
 |
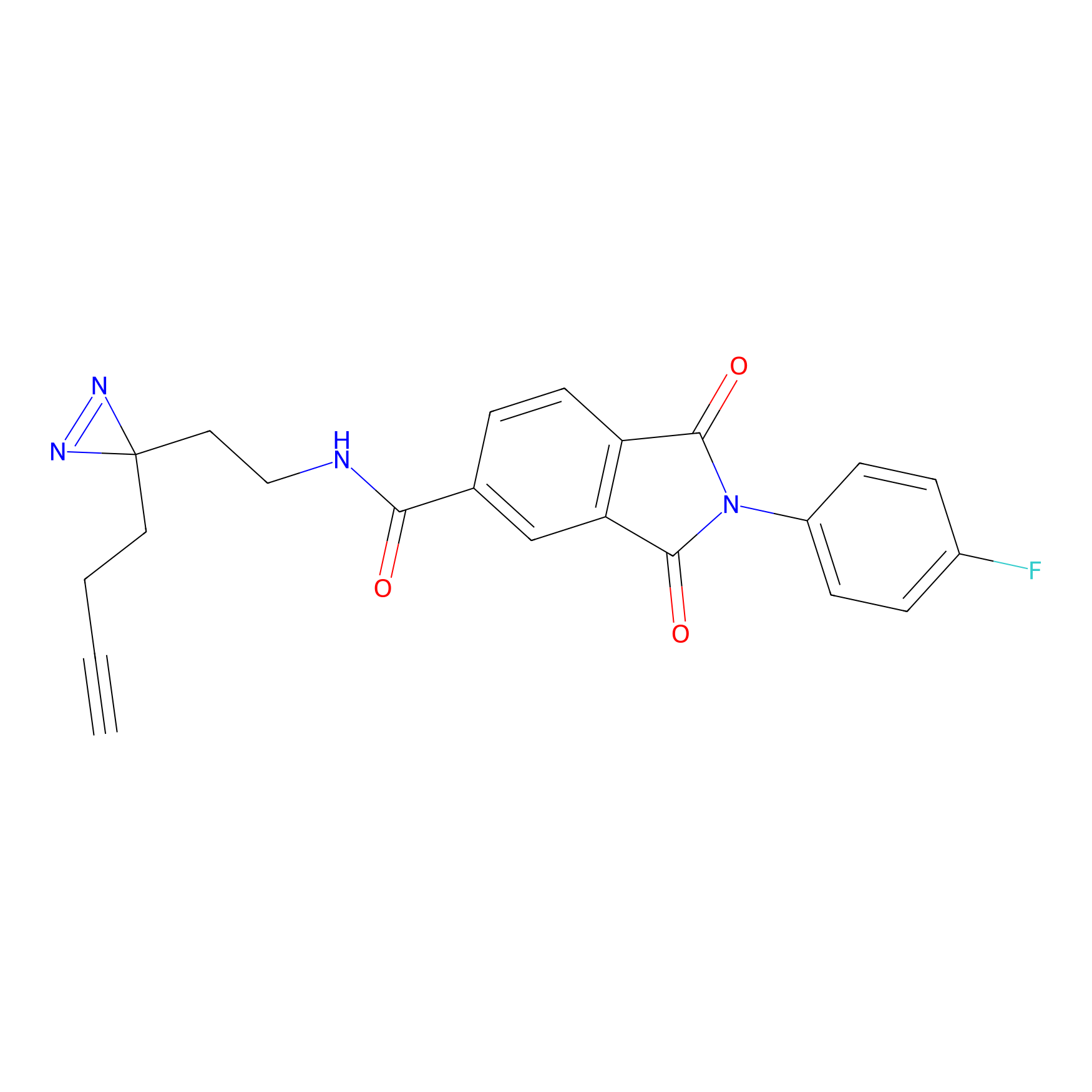
C346(5.16) | LDD2184 | [1] | |
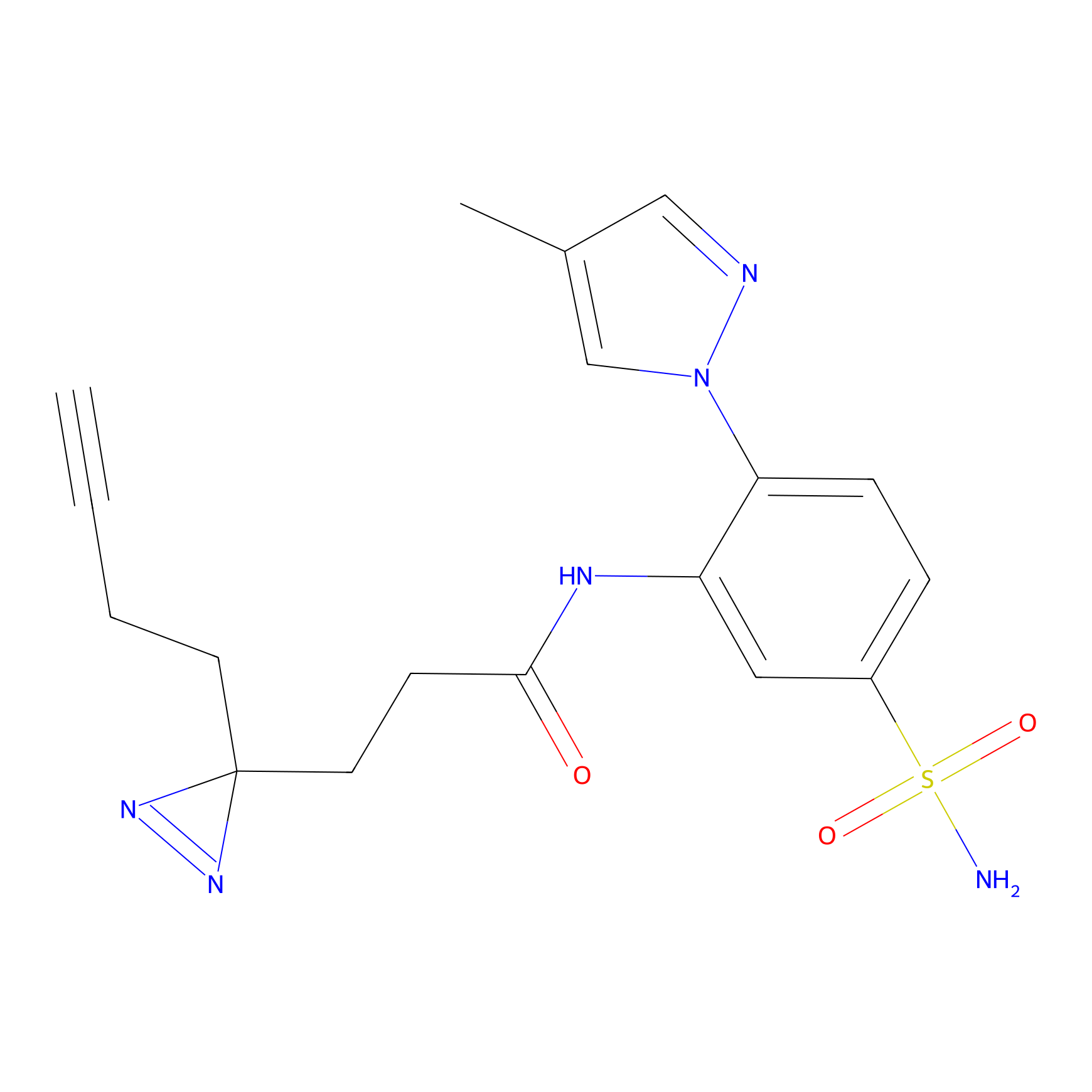
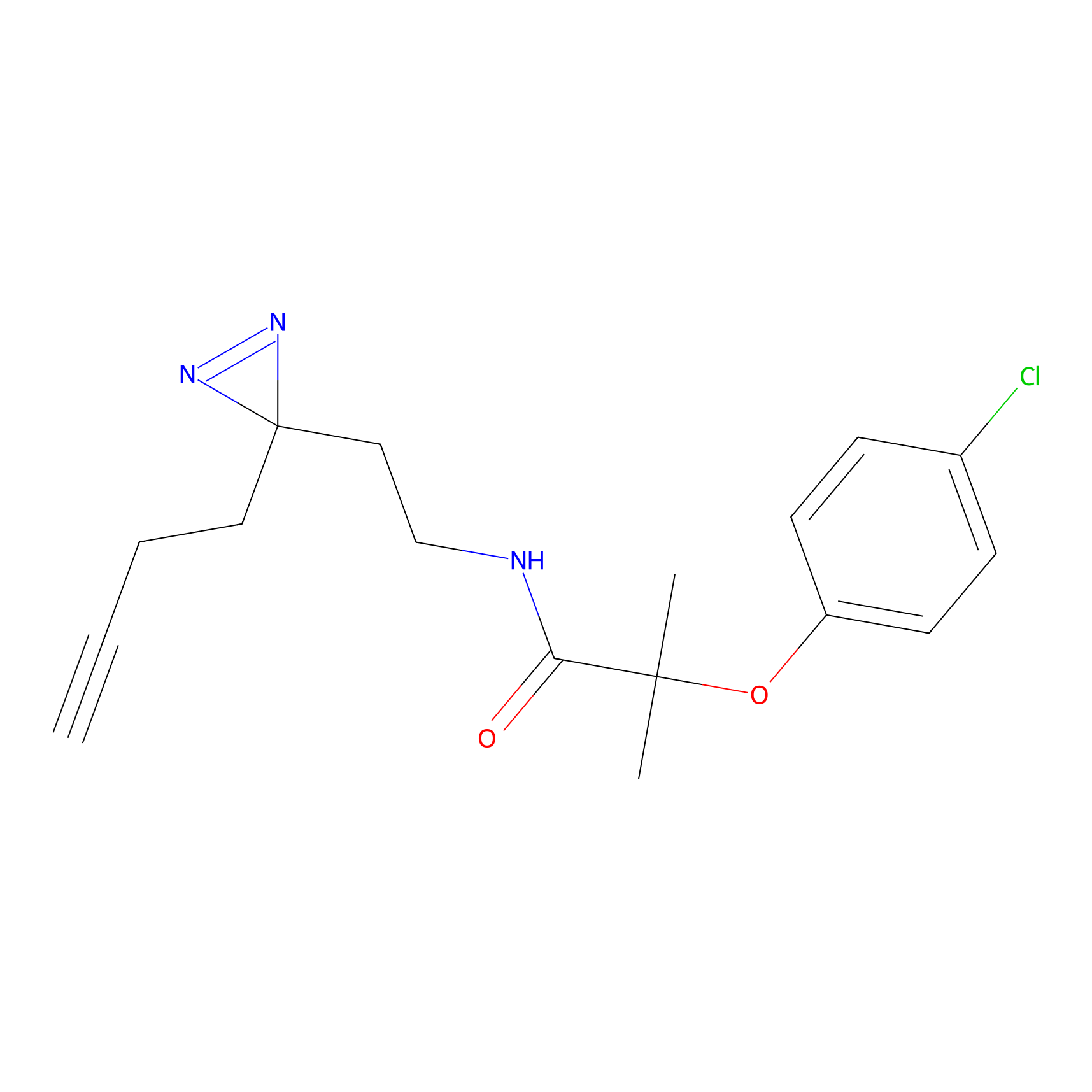
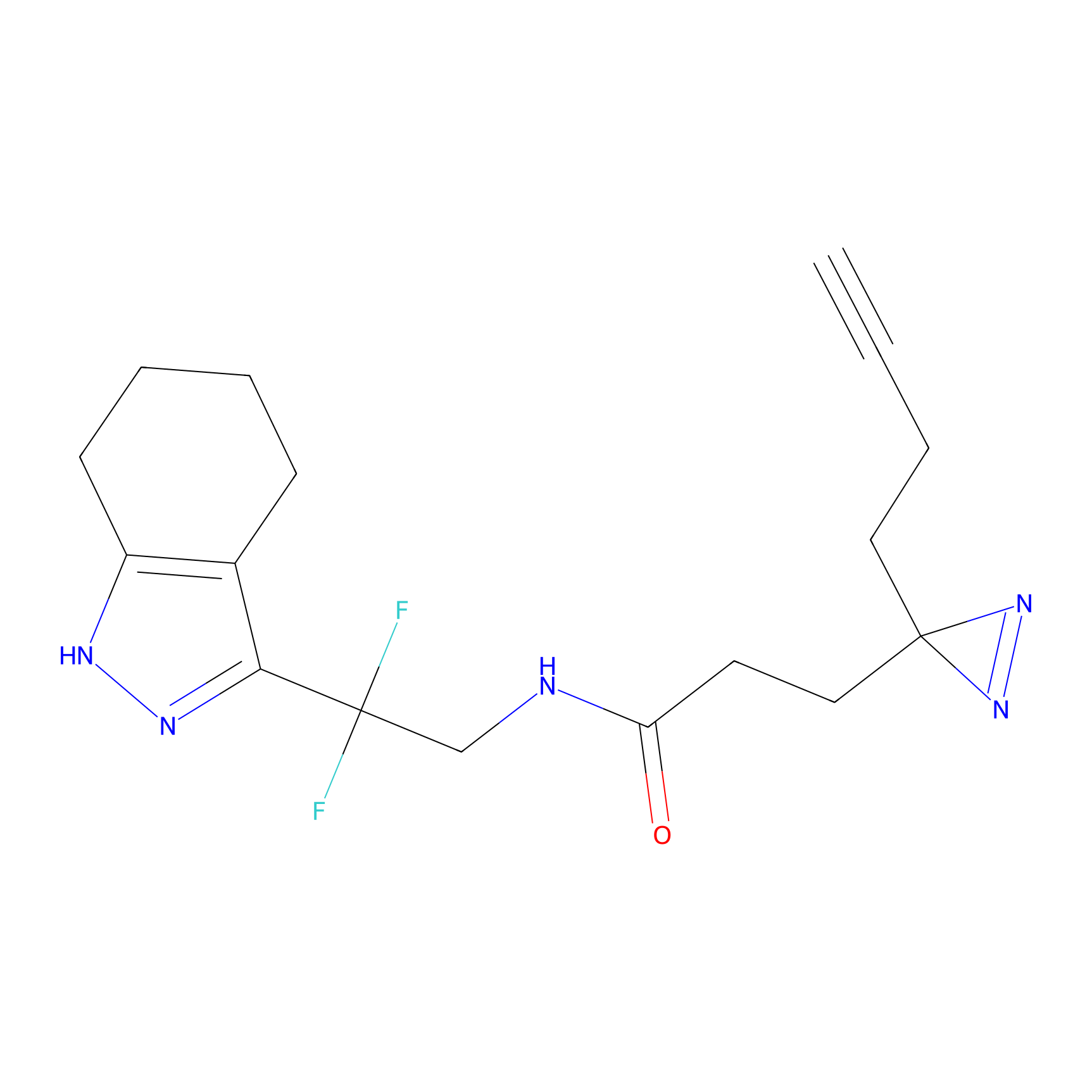
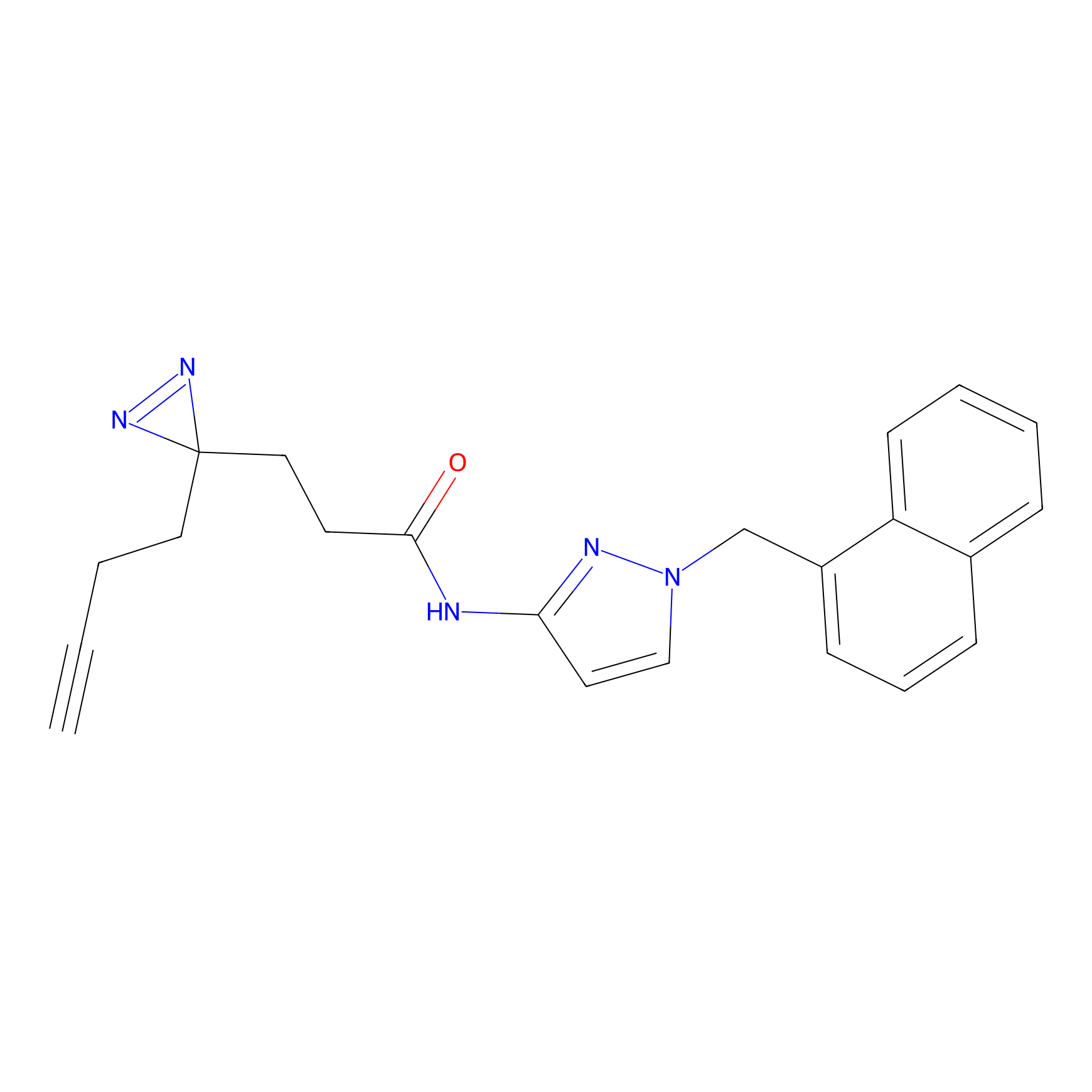
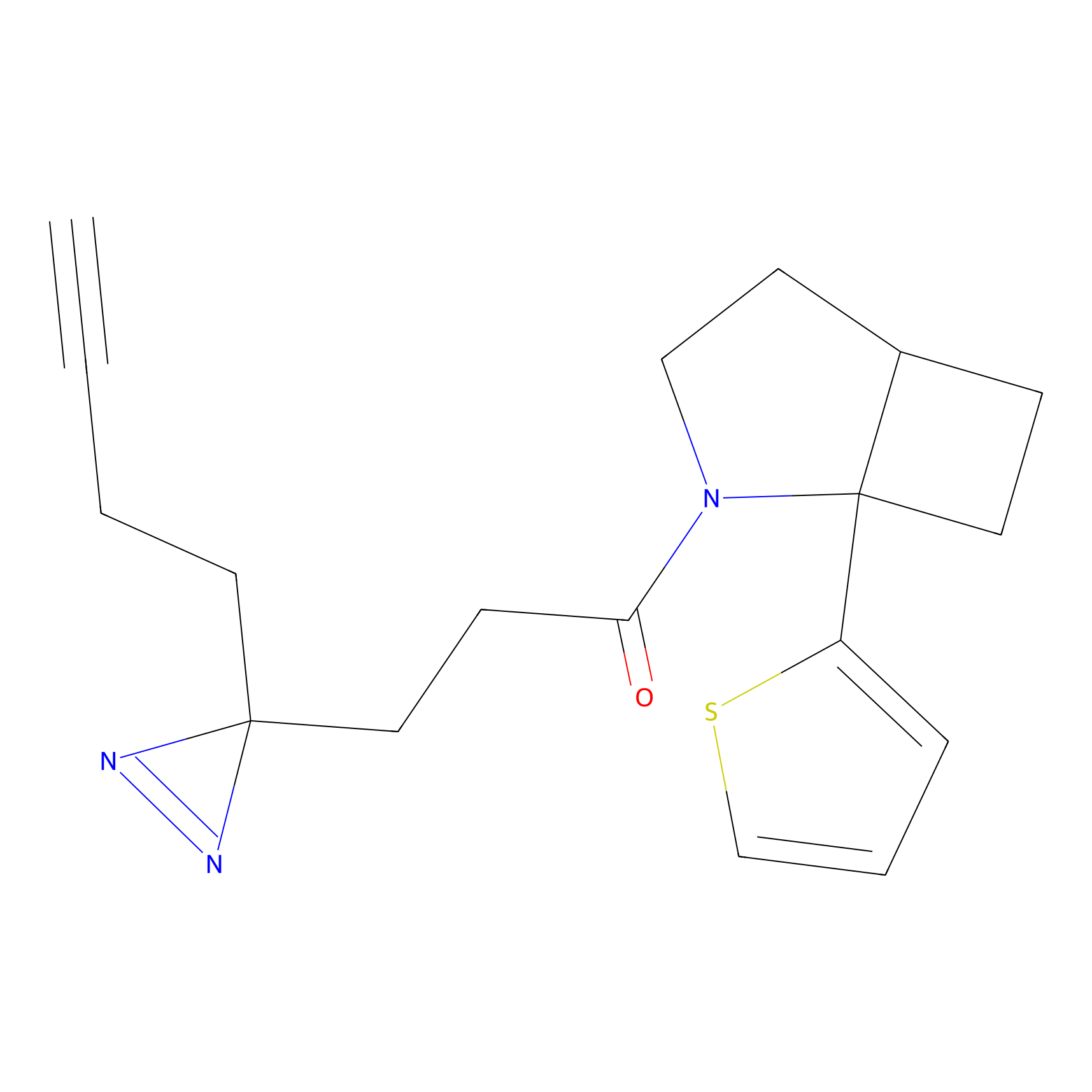
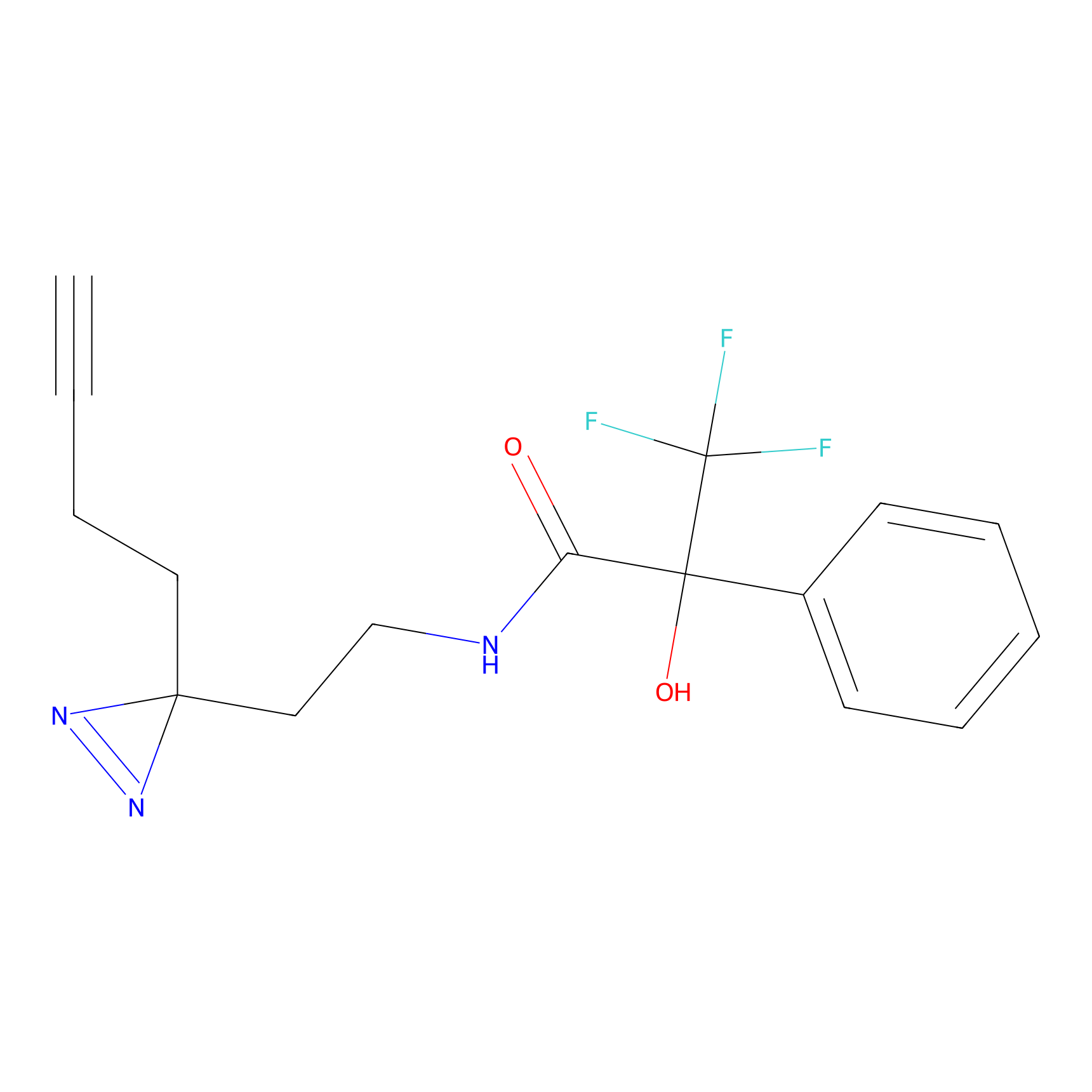
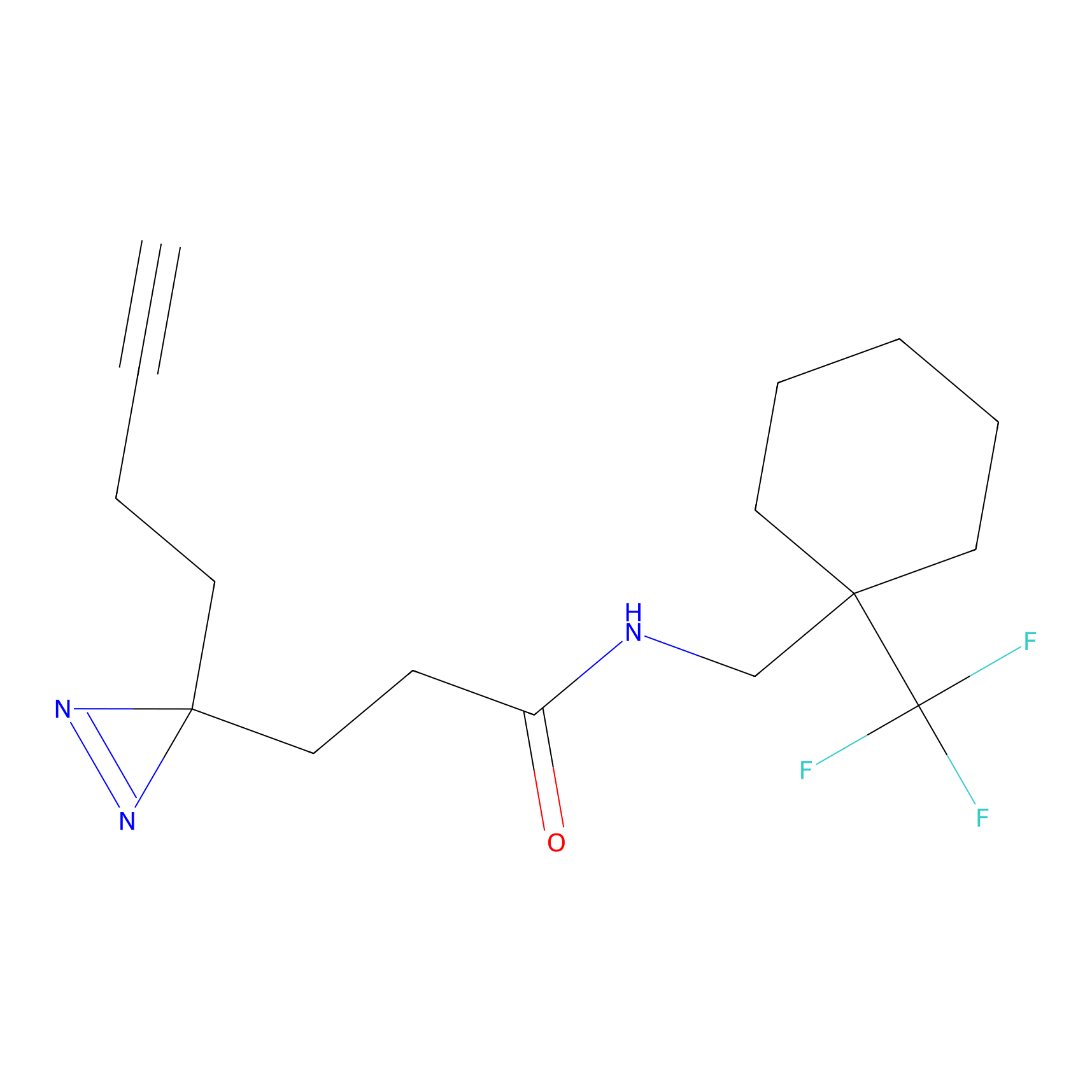
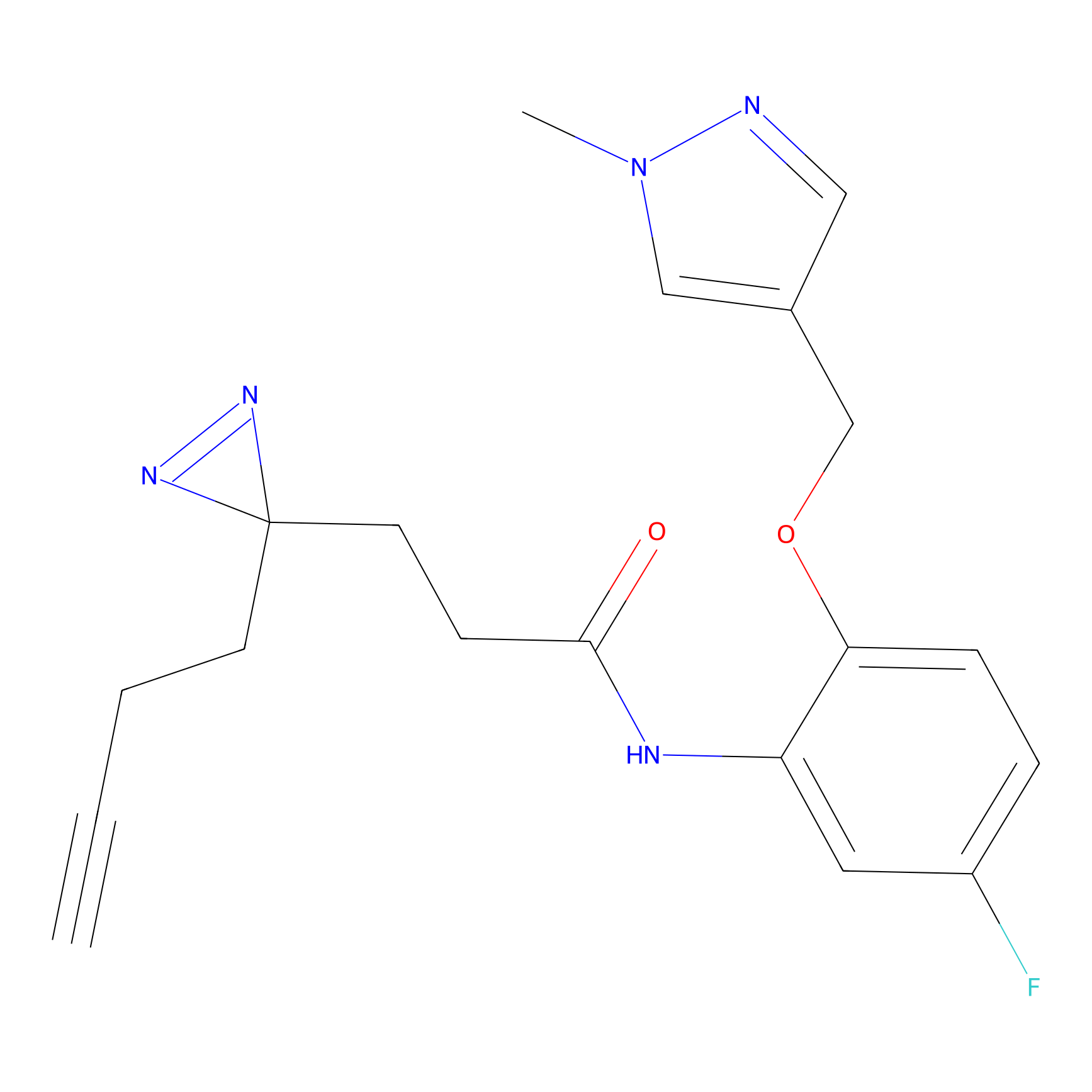
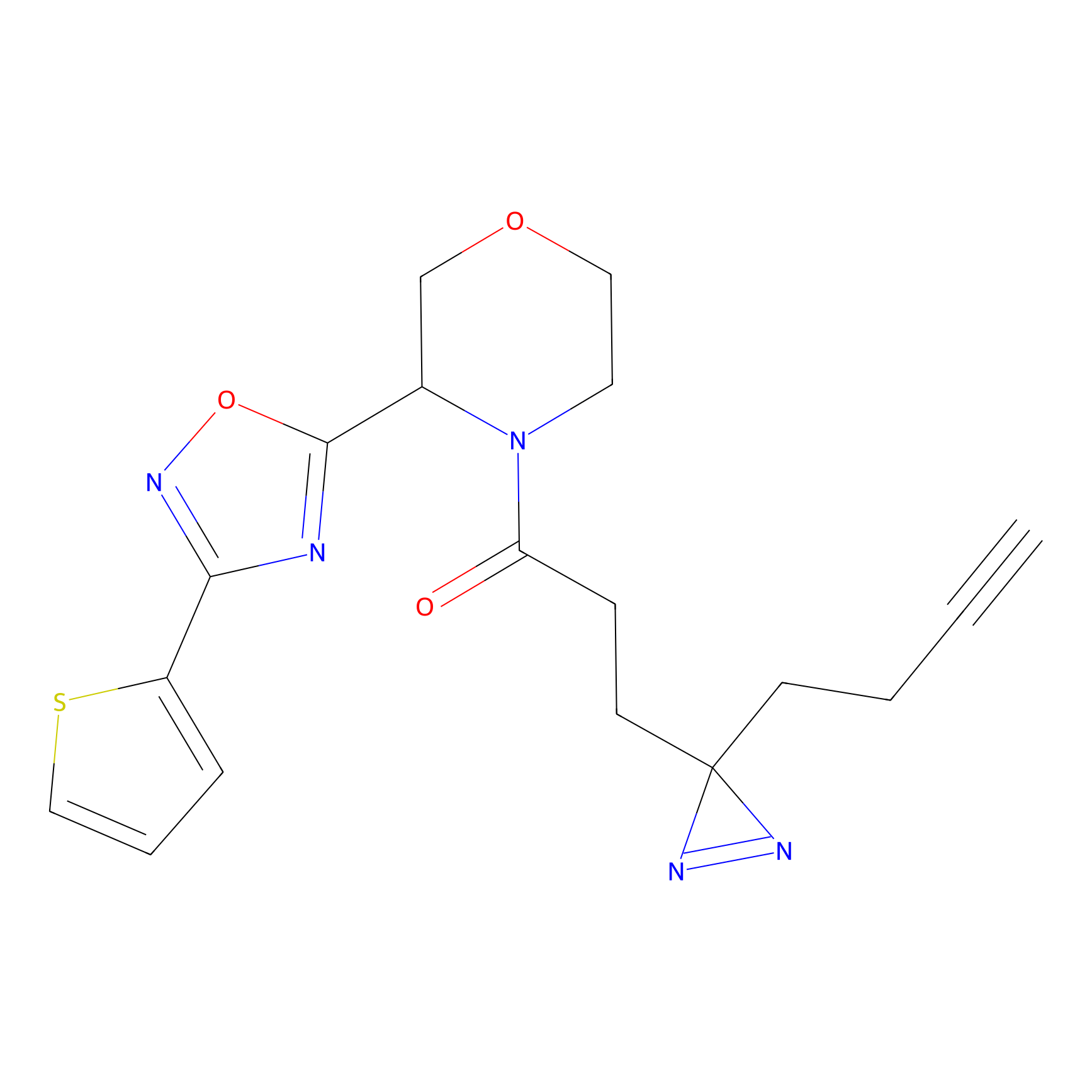
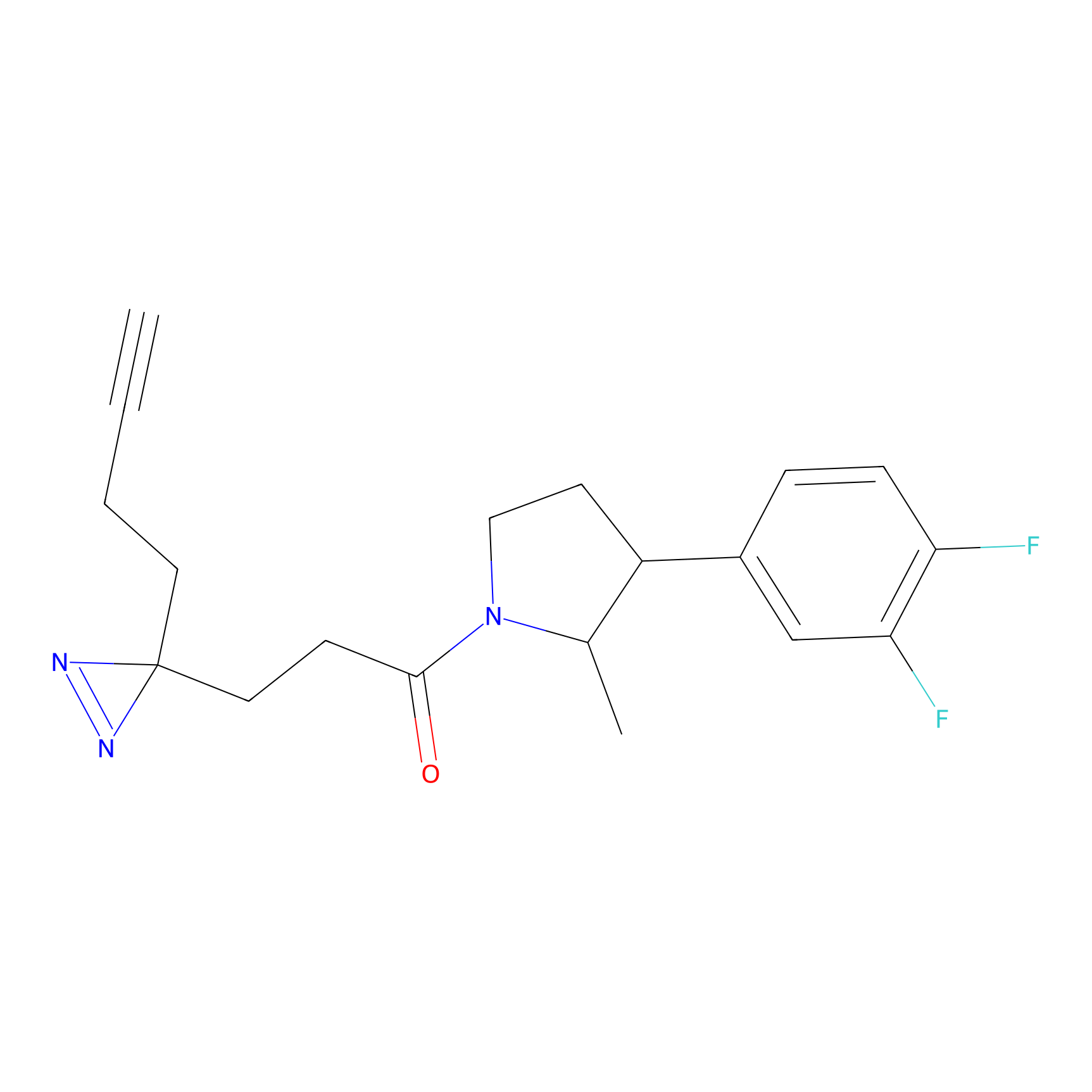
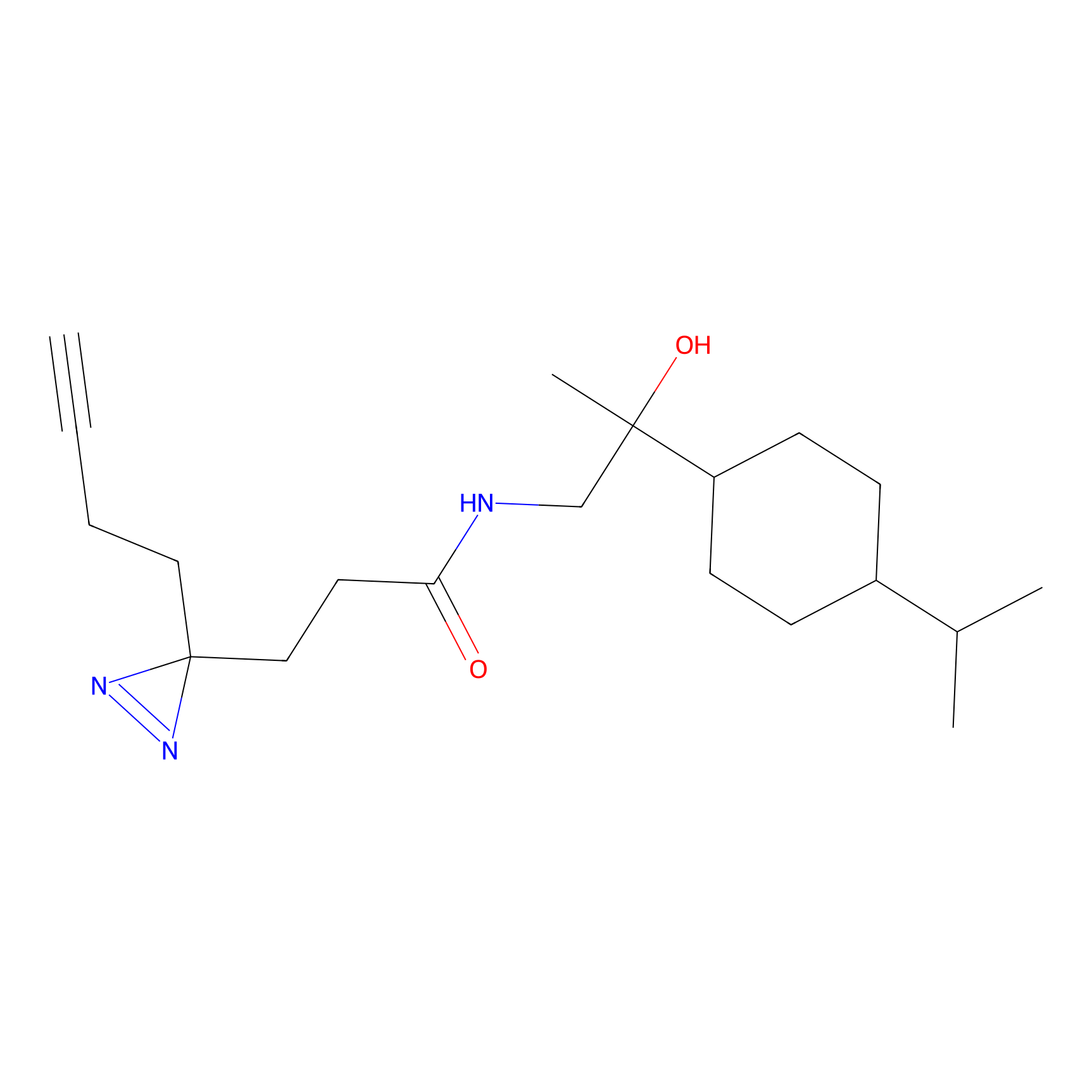
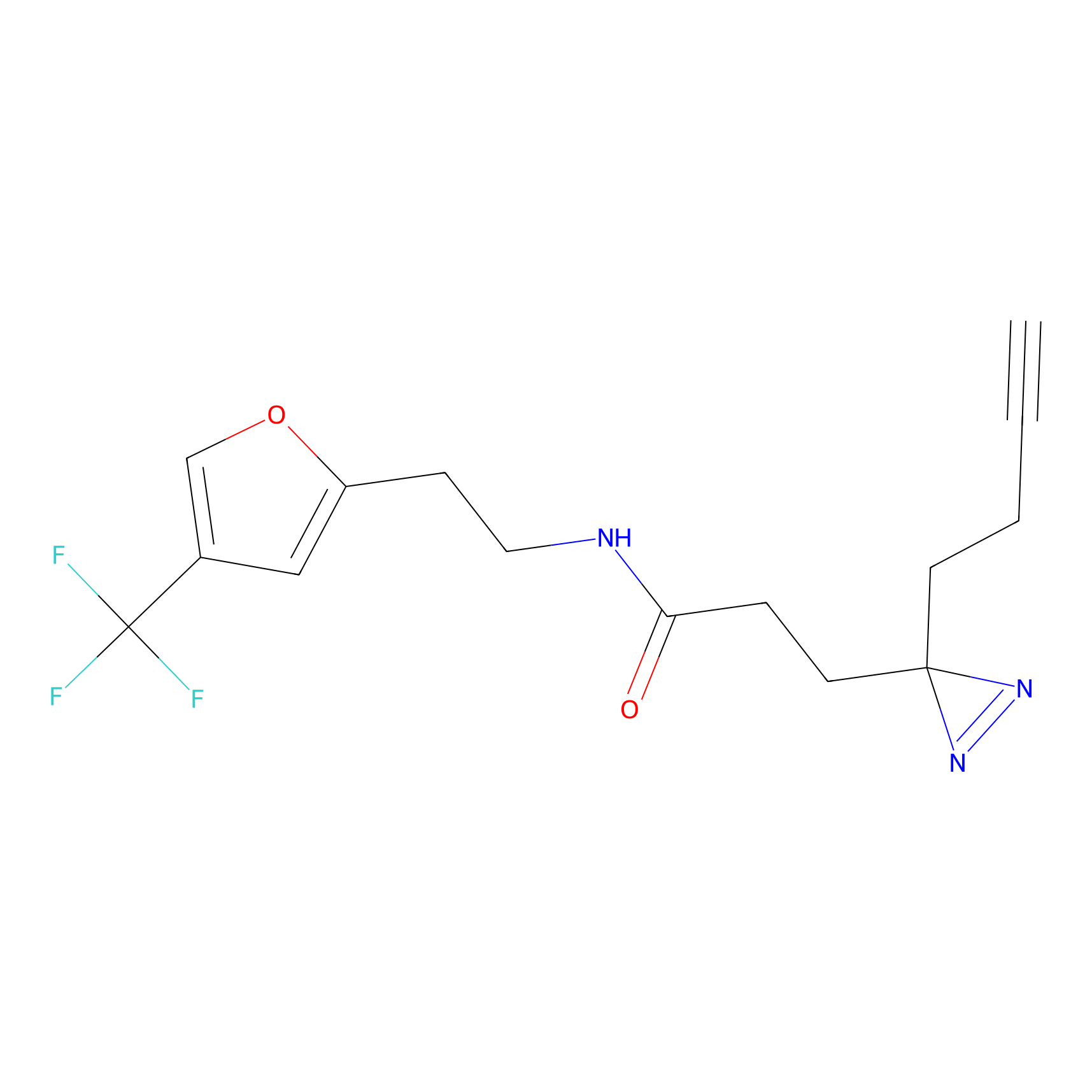
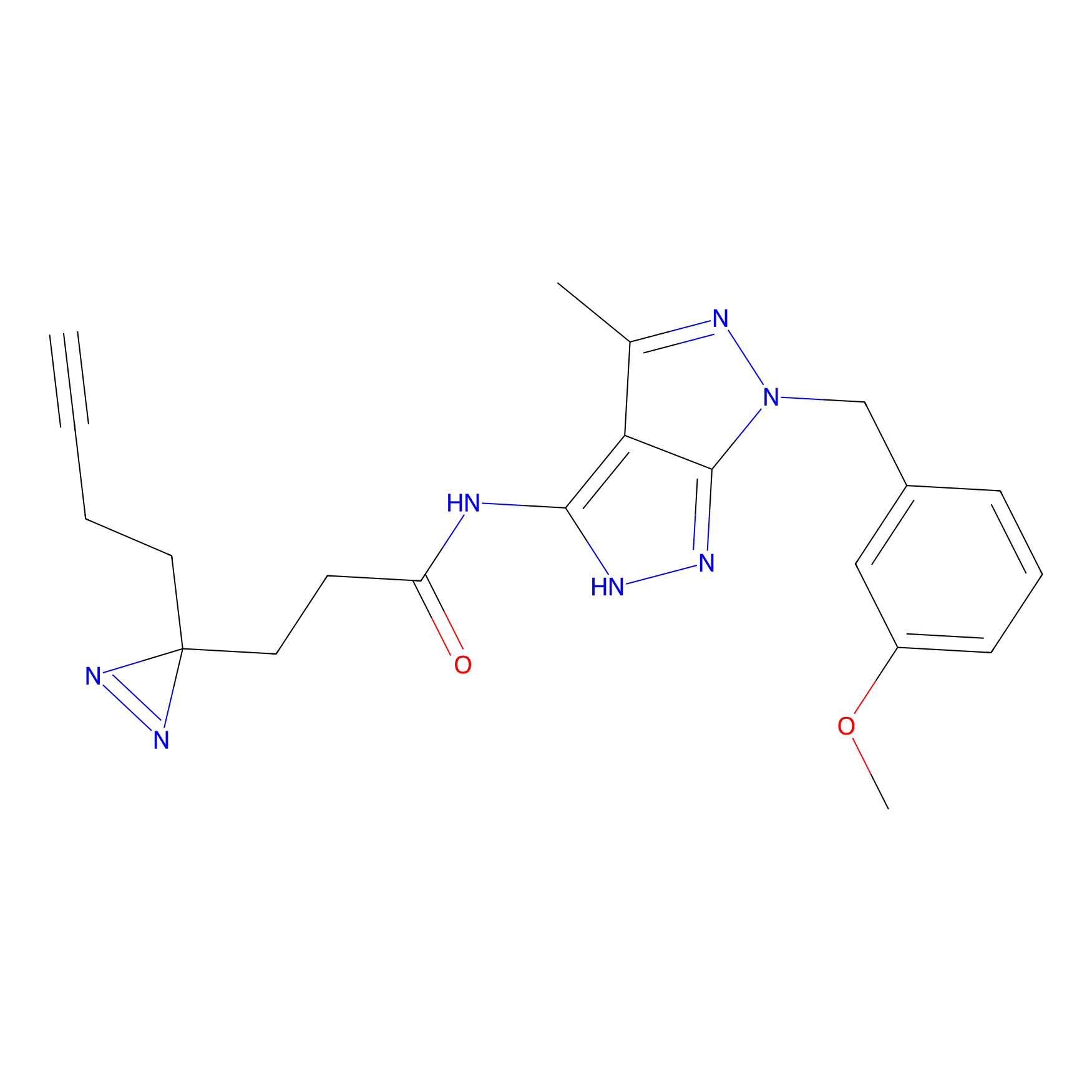
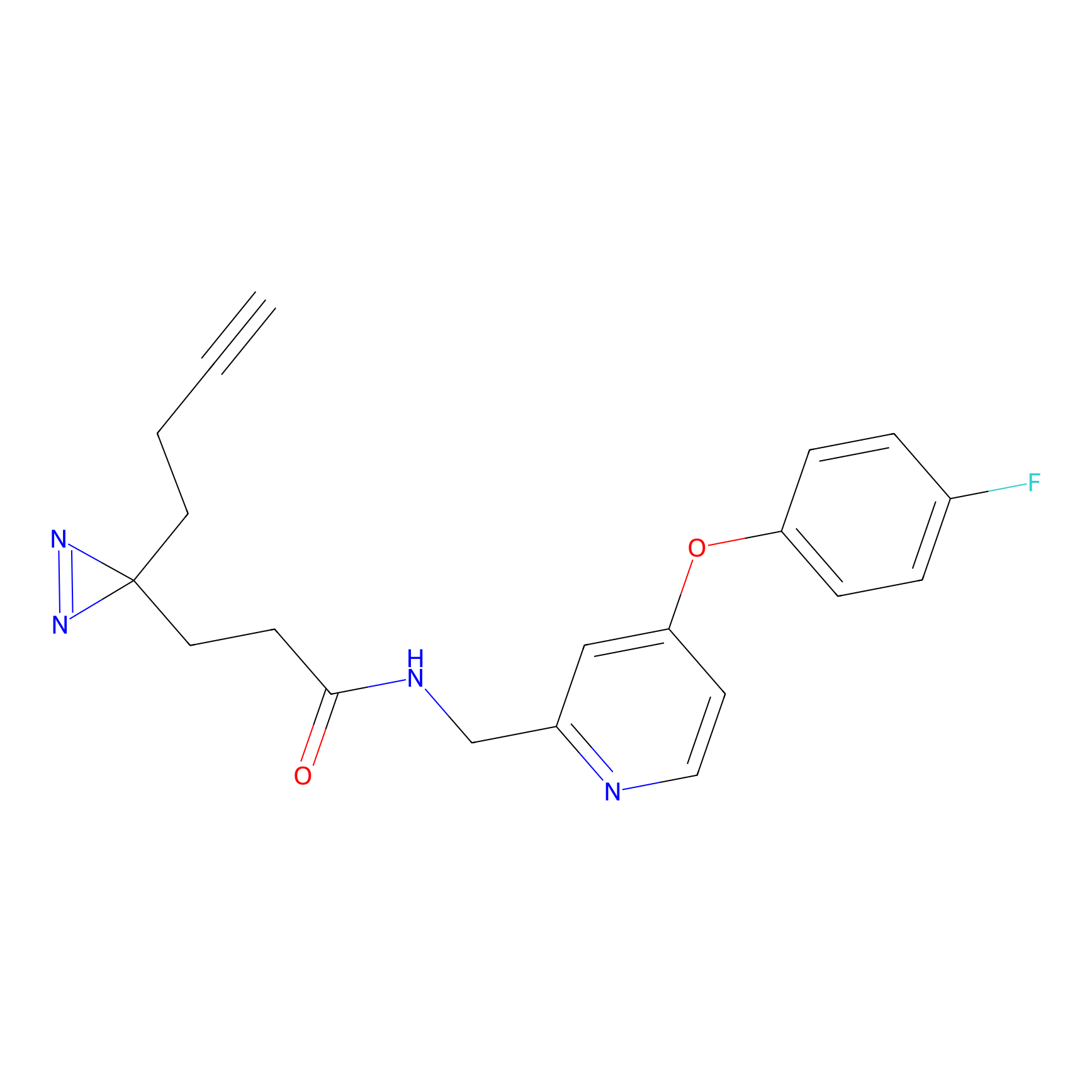
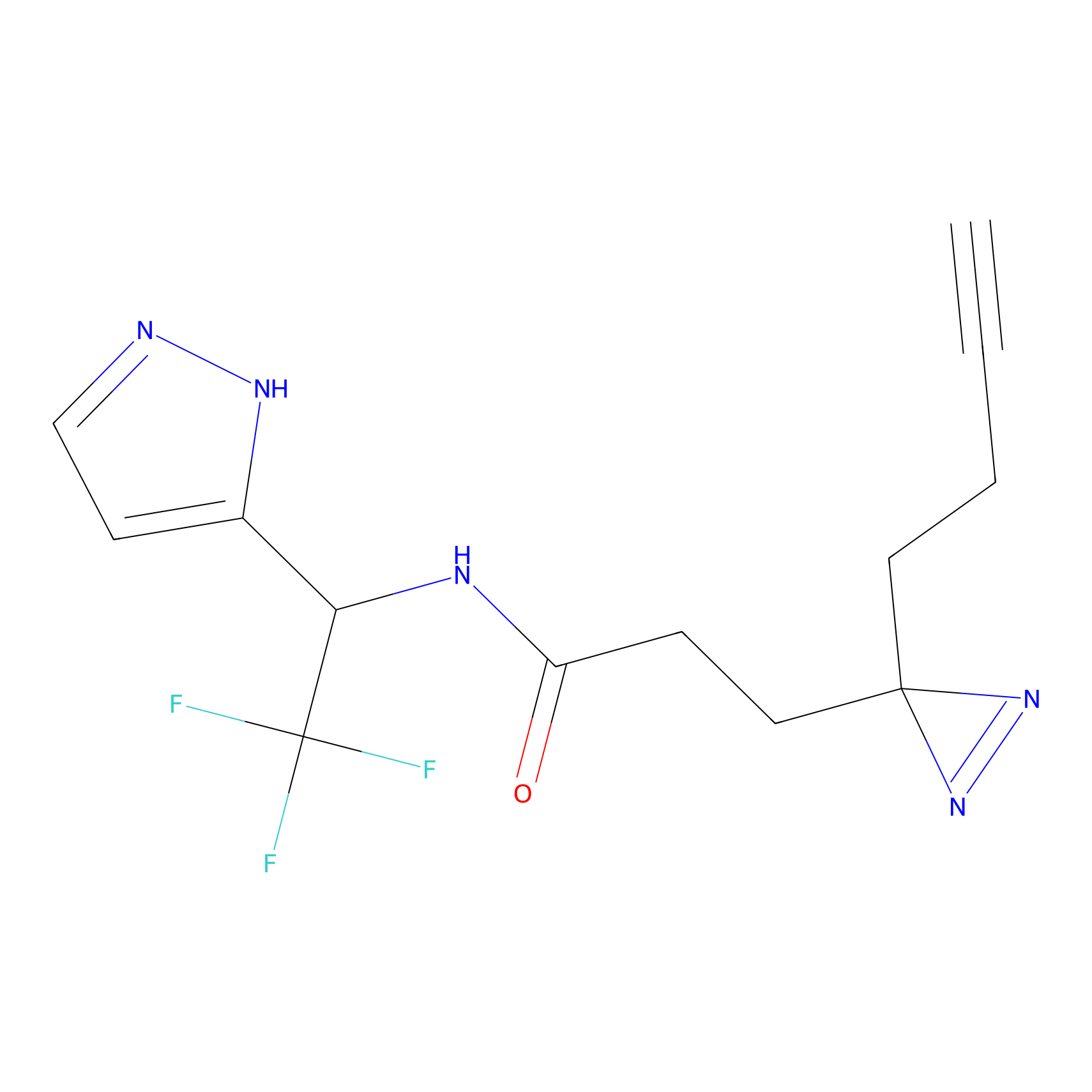
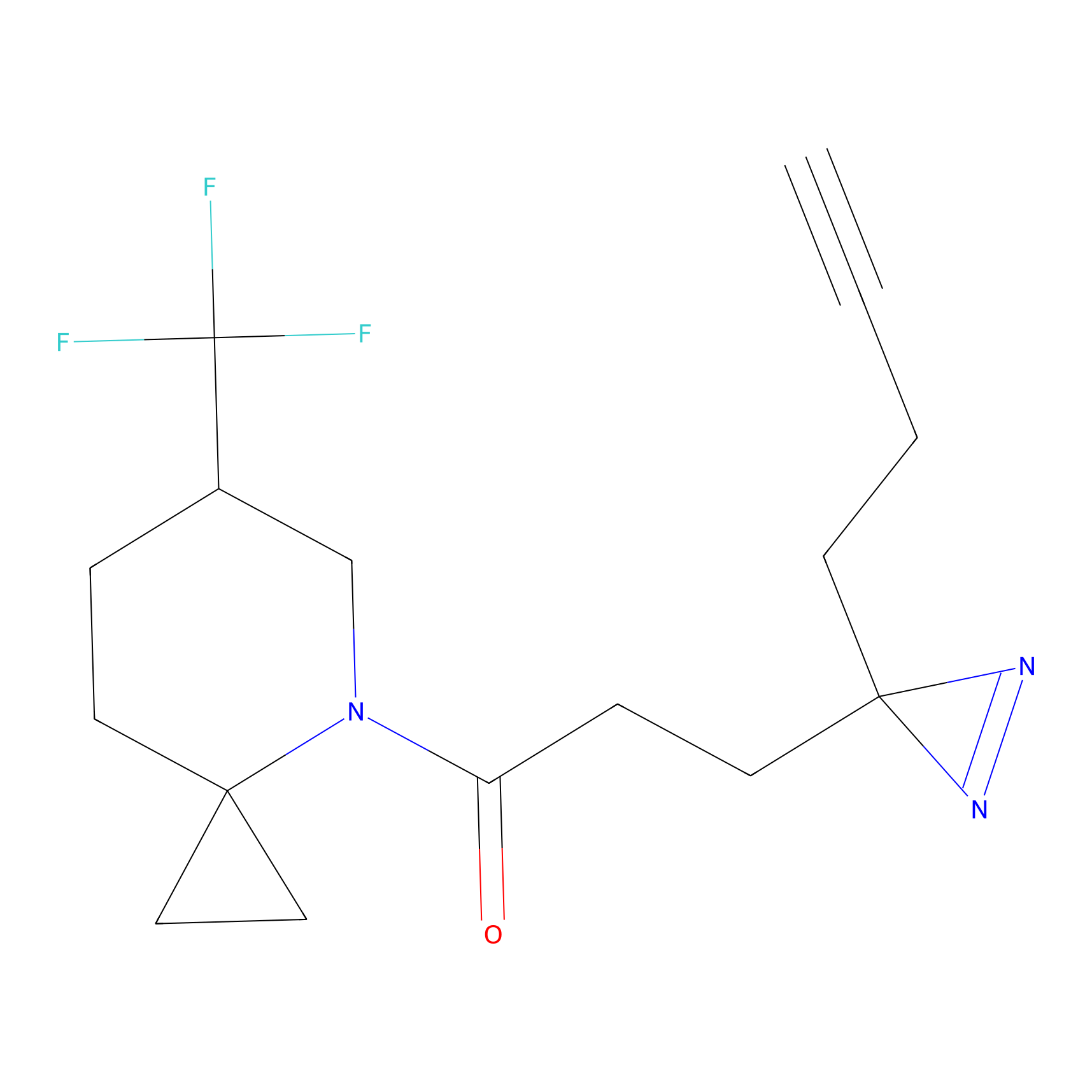
|
DBIA Probe Info |
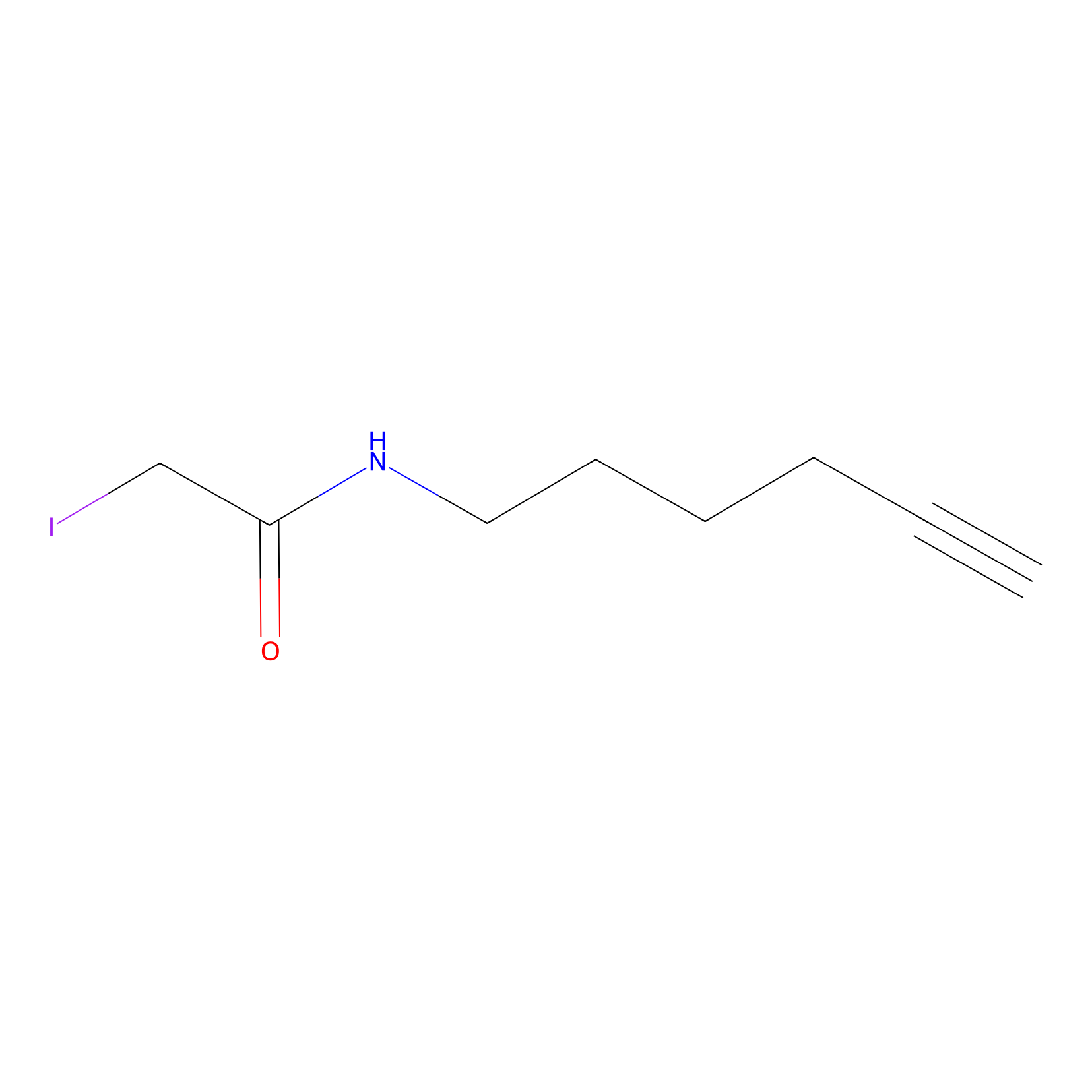
 |
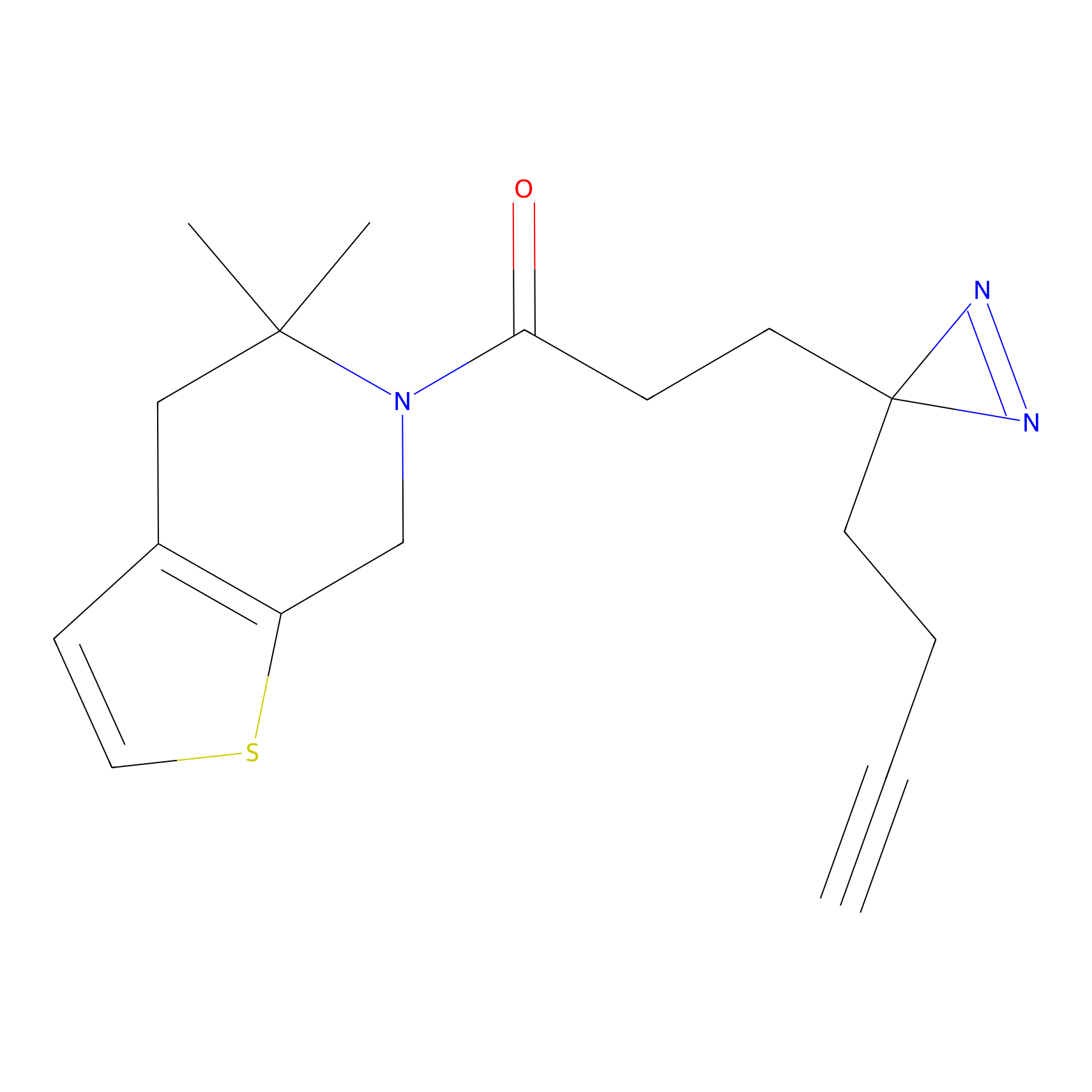
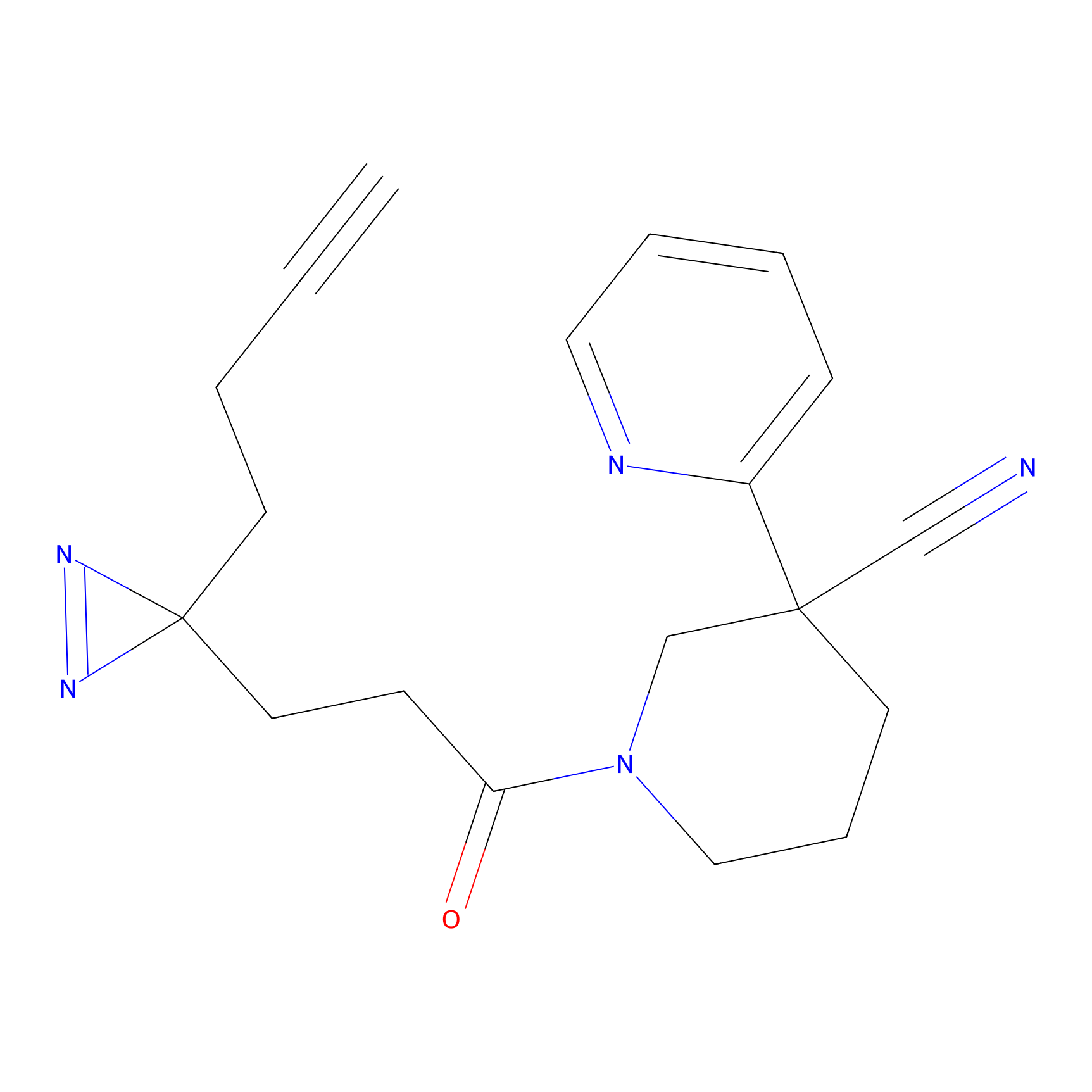
C296(0.92) | LDD1511 | [2] | |
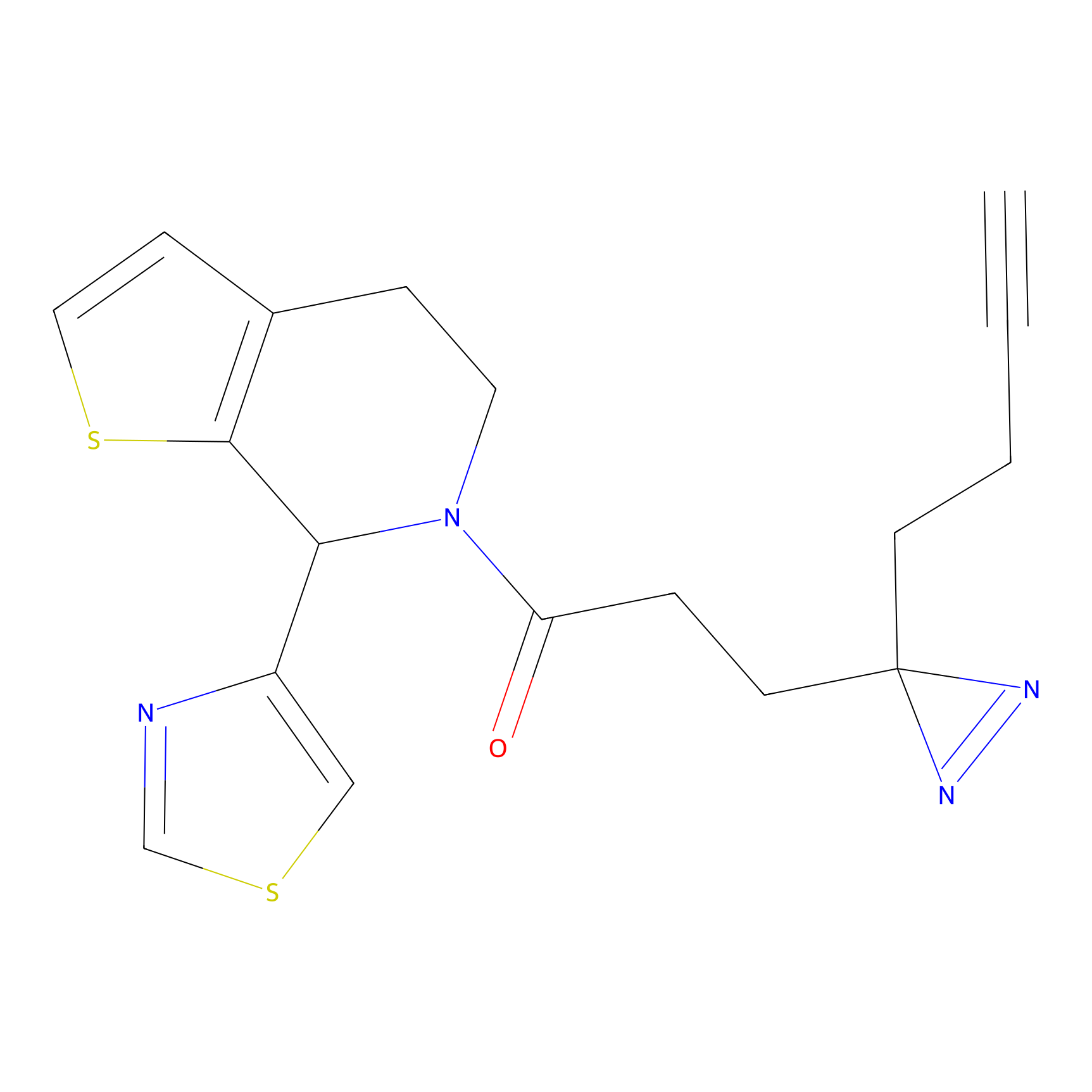
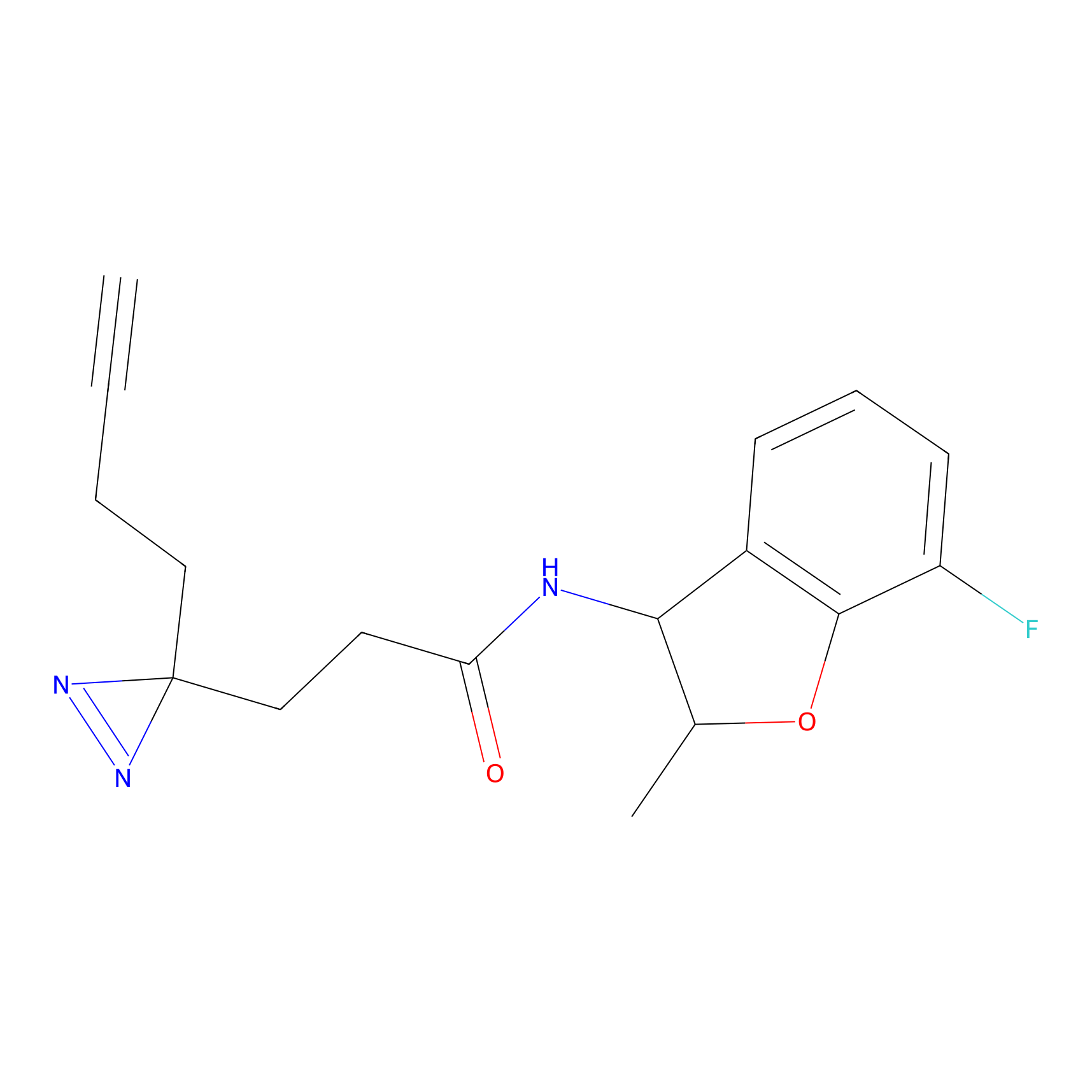
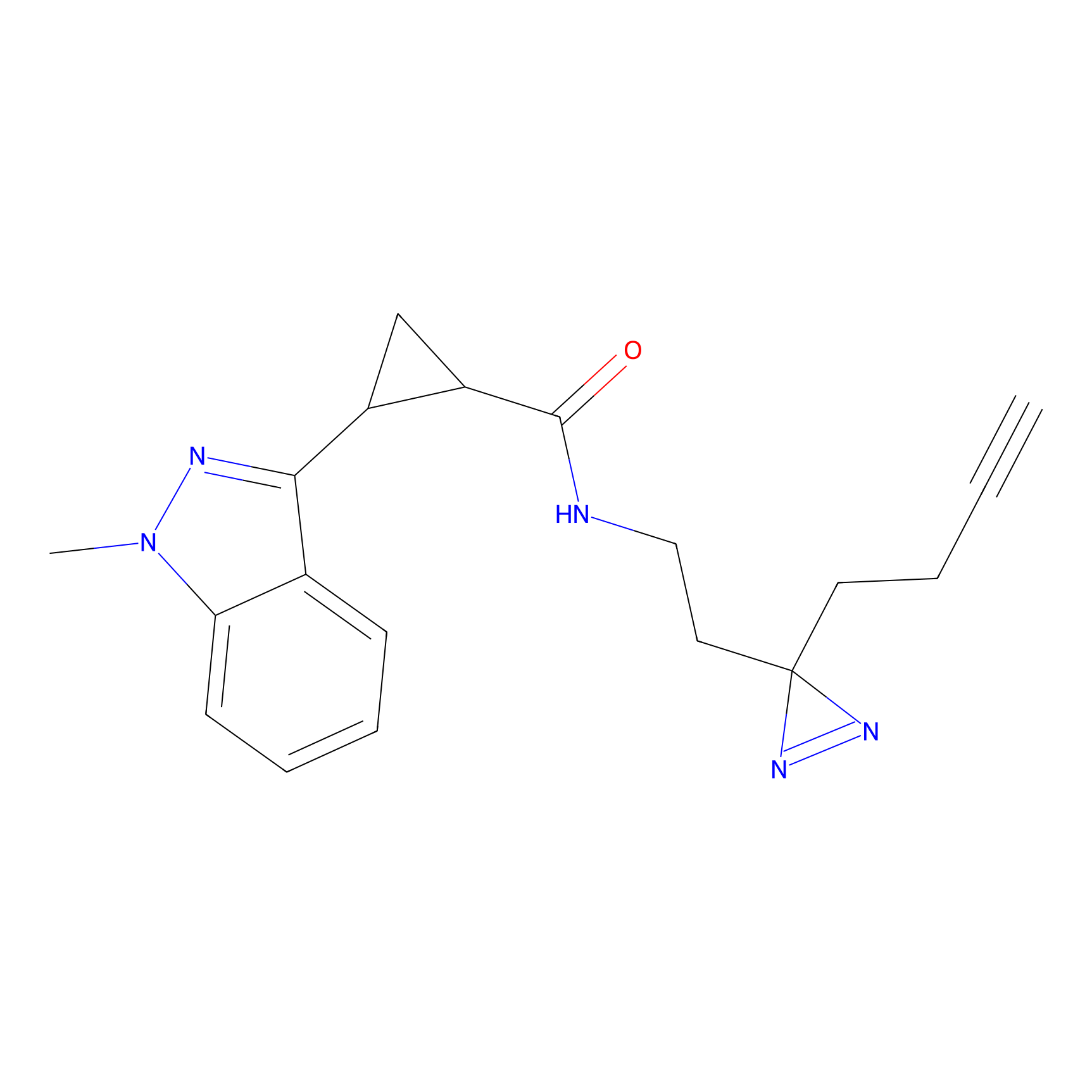
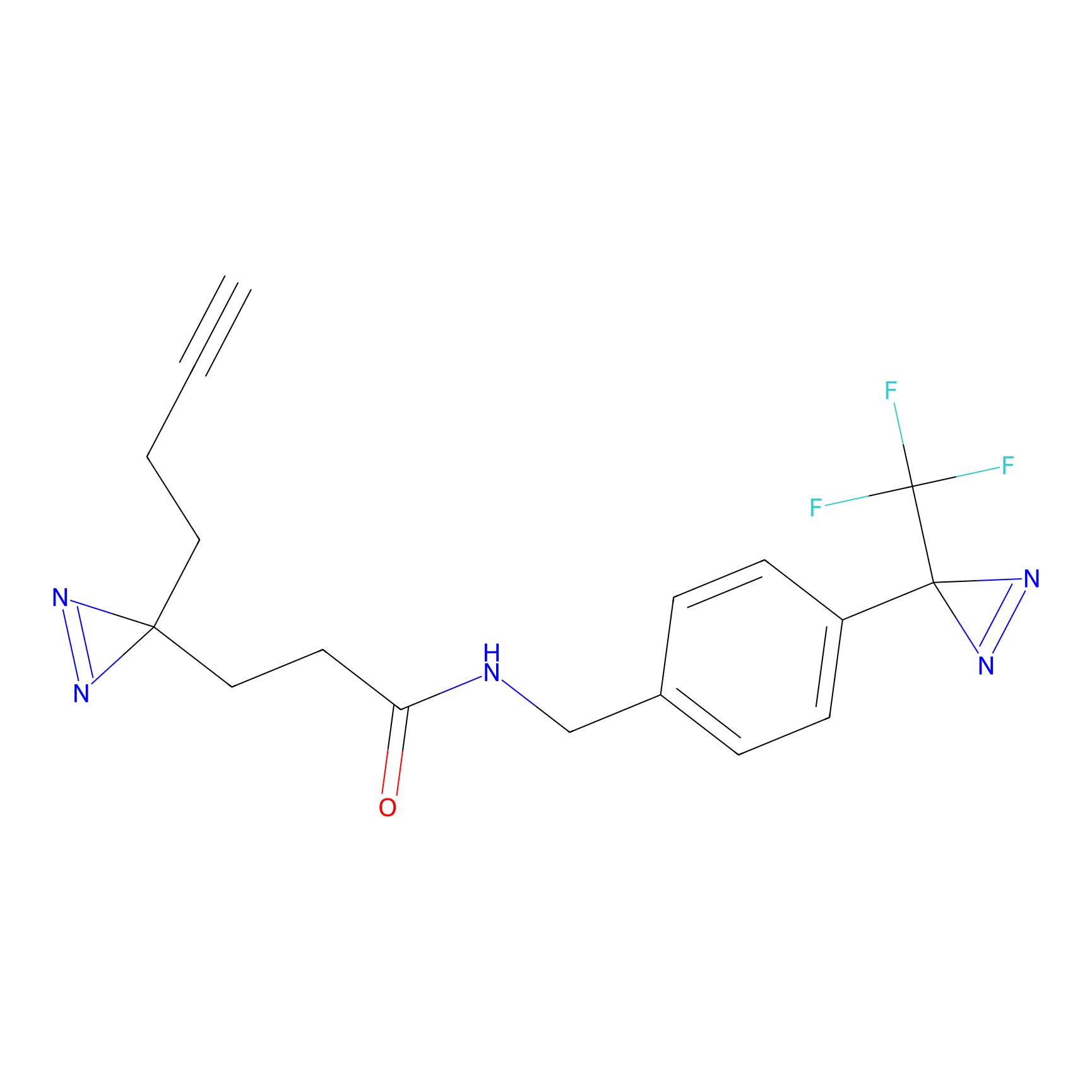
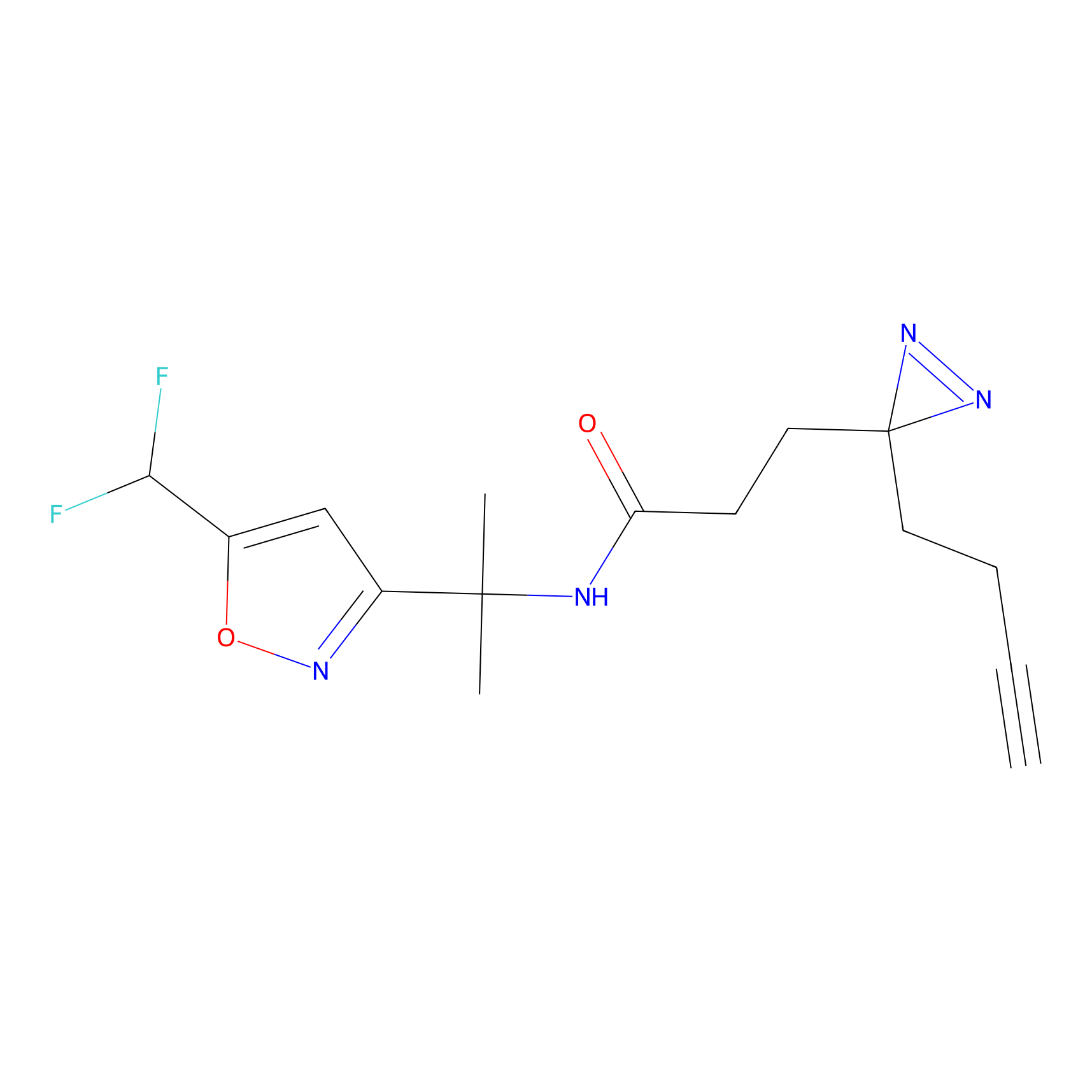
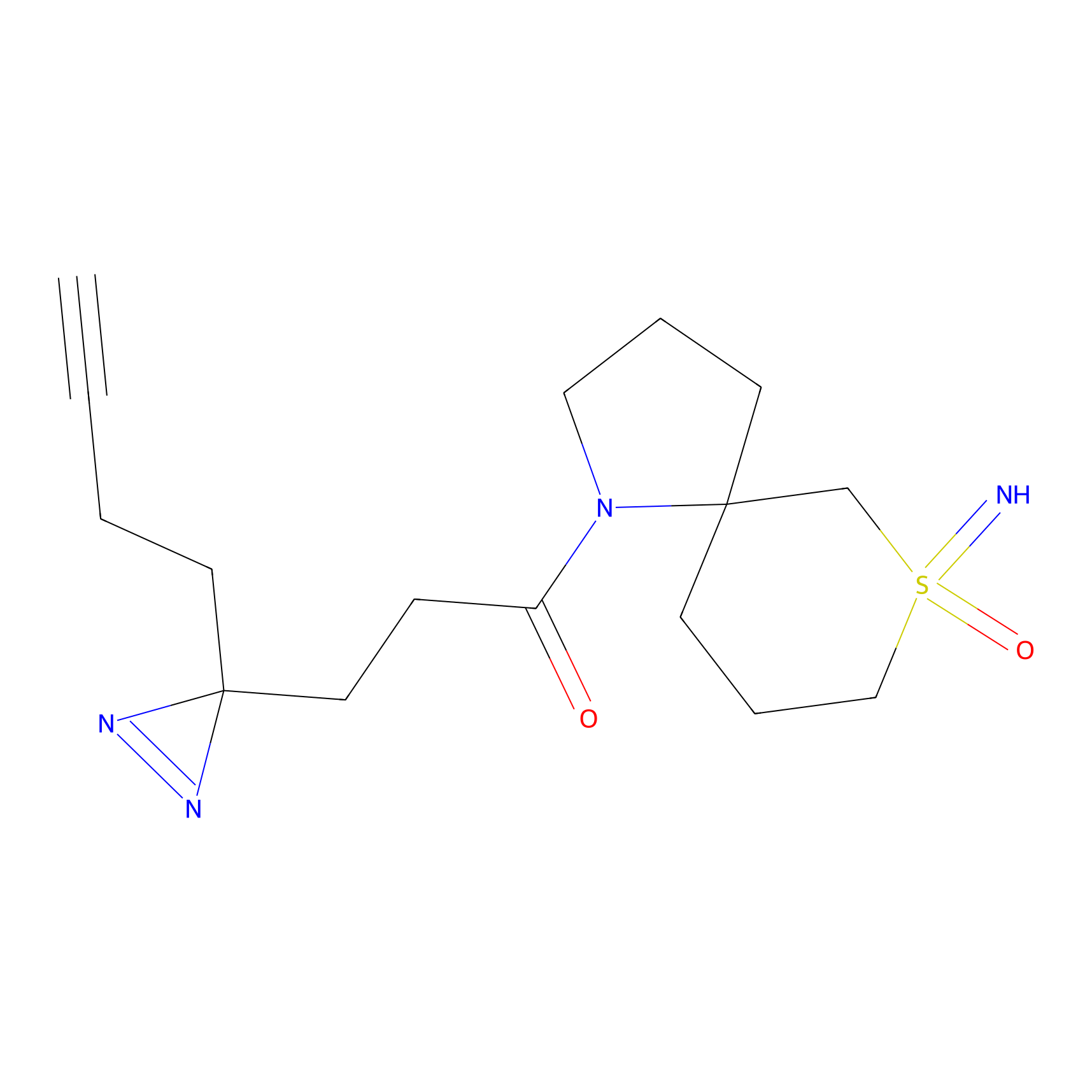
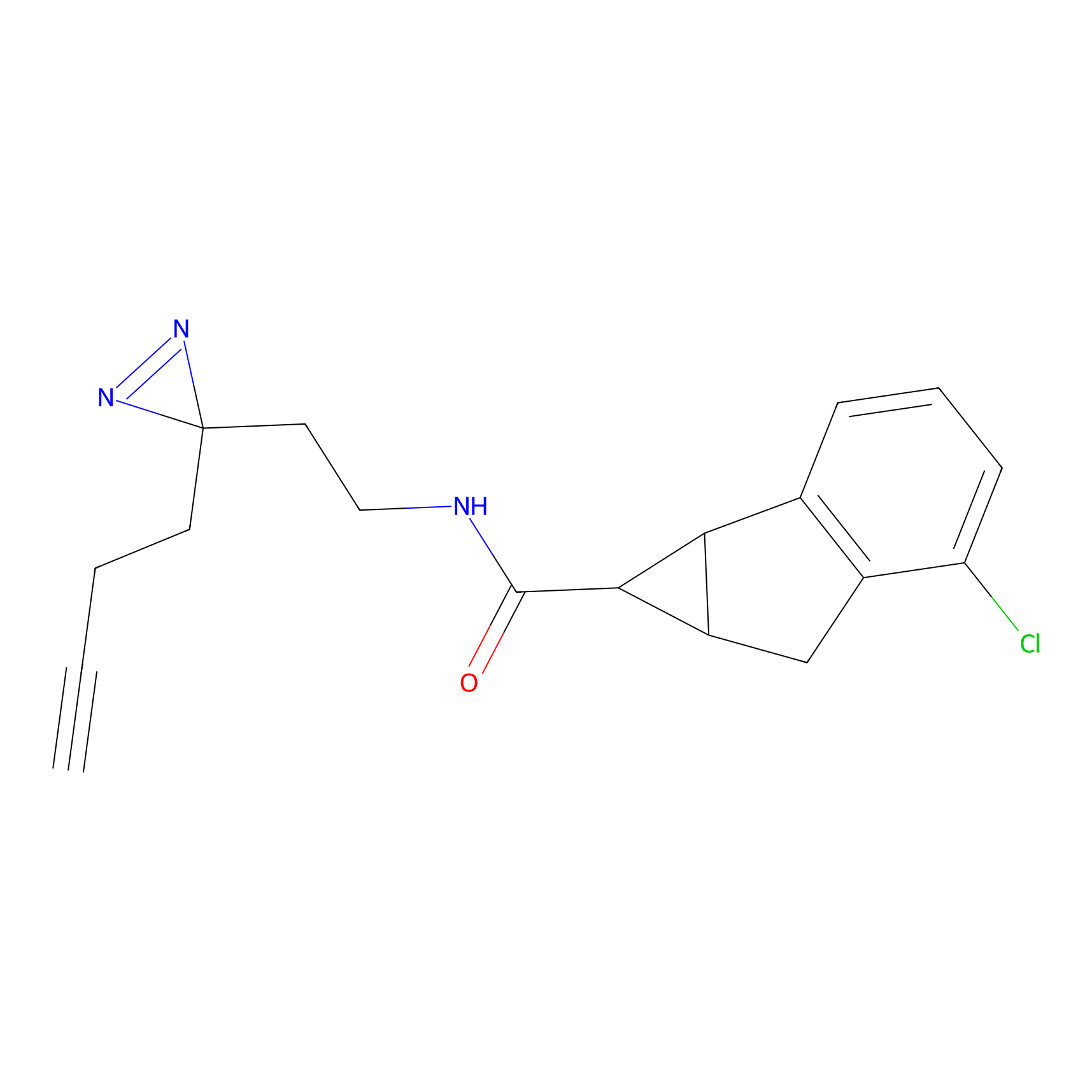
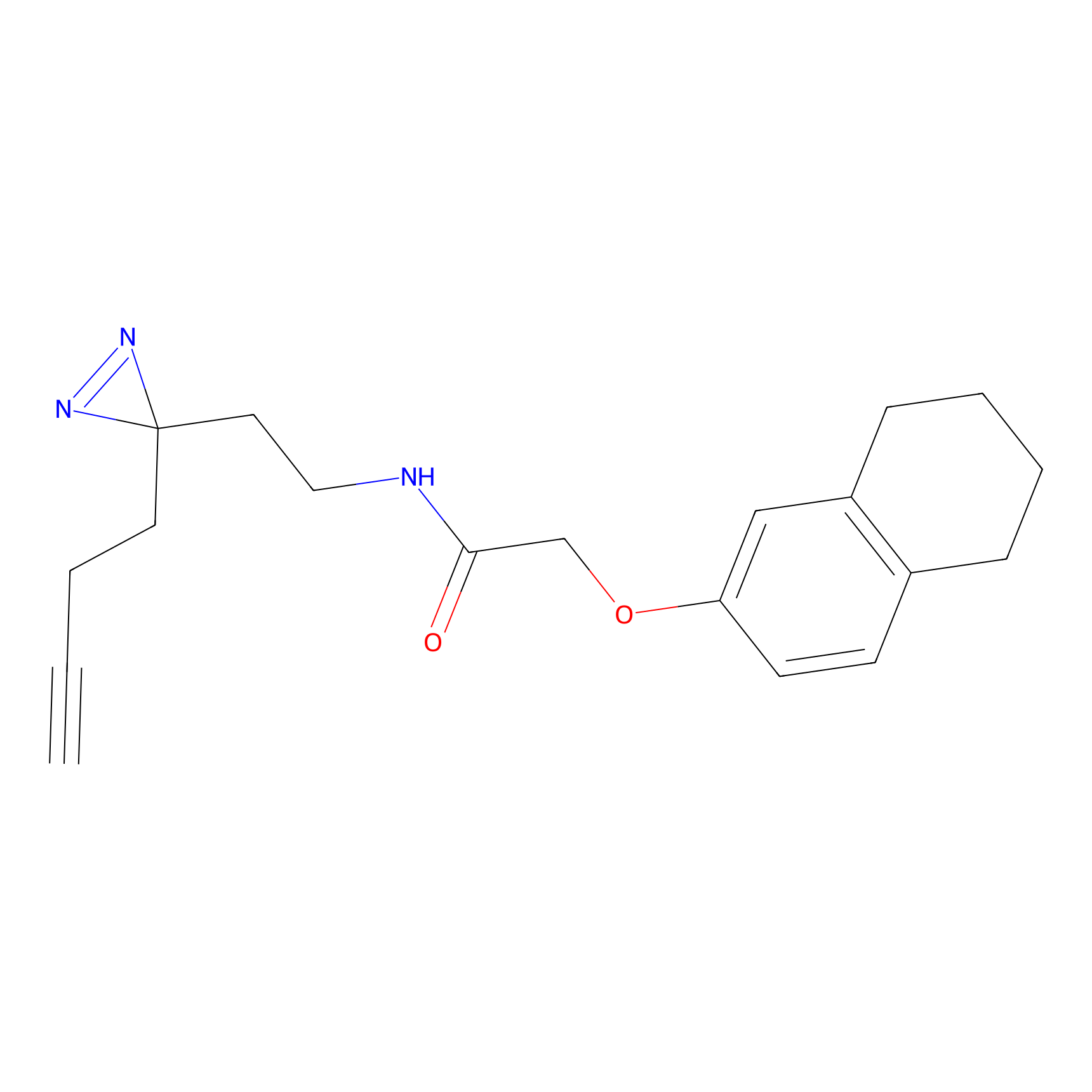
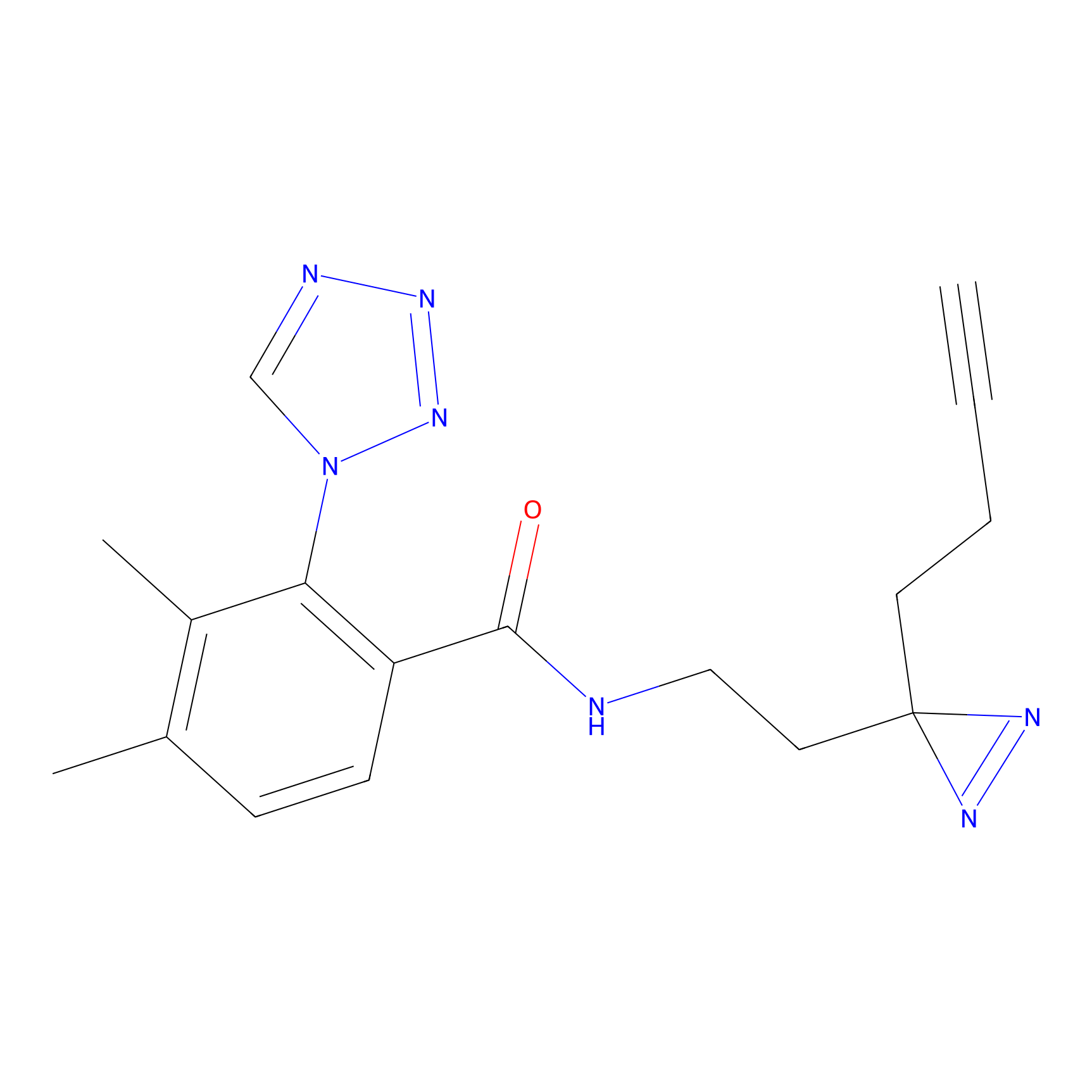
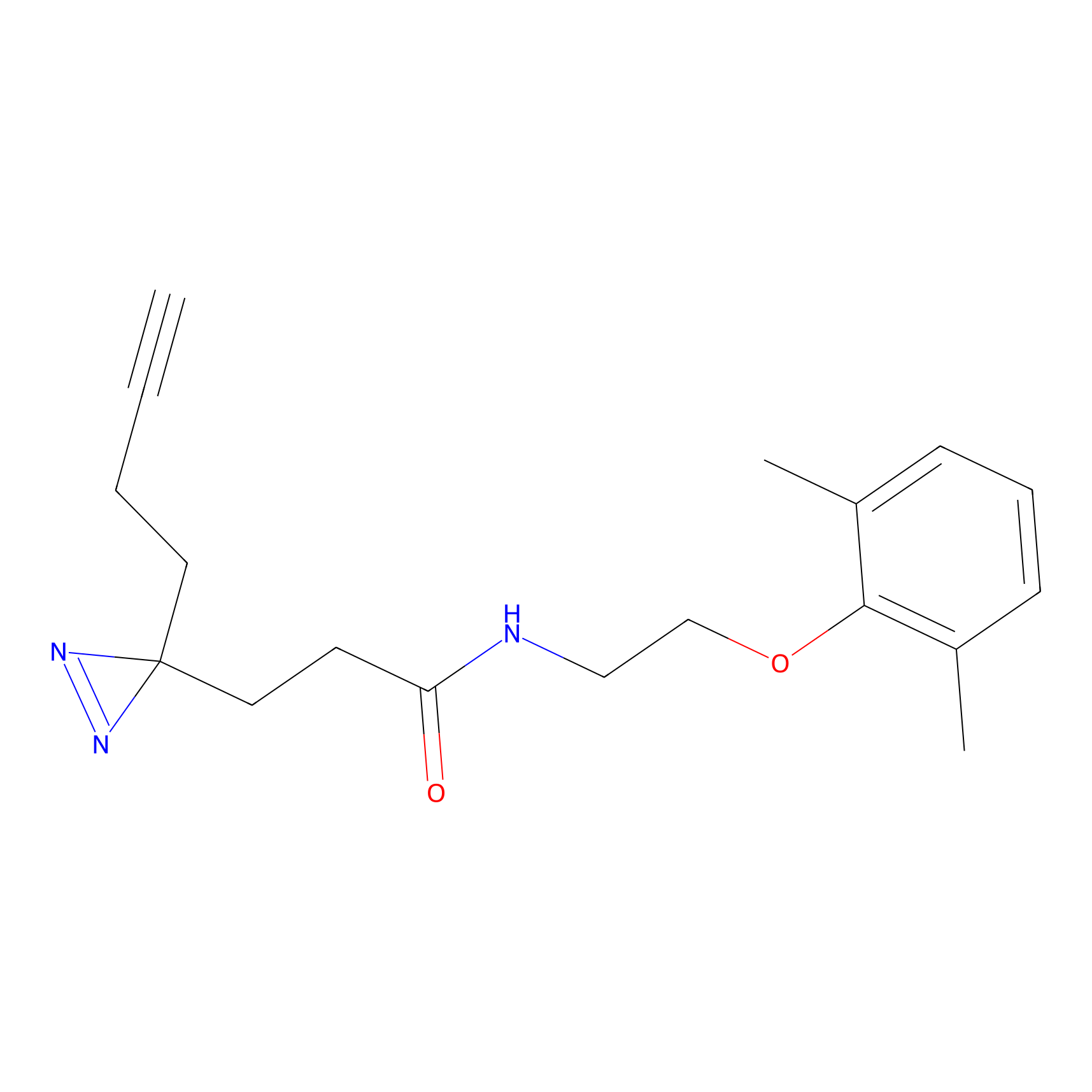
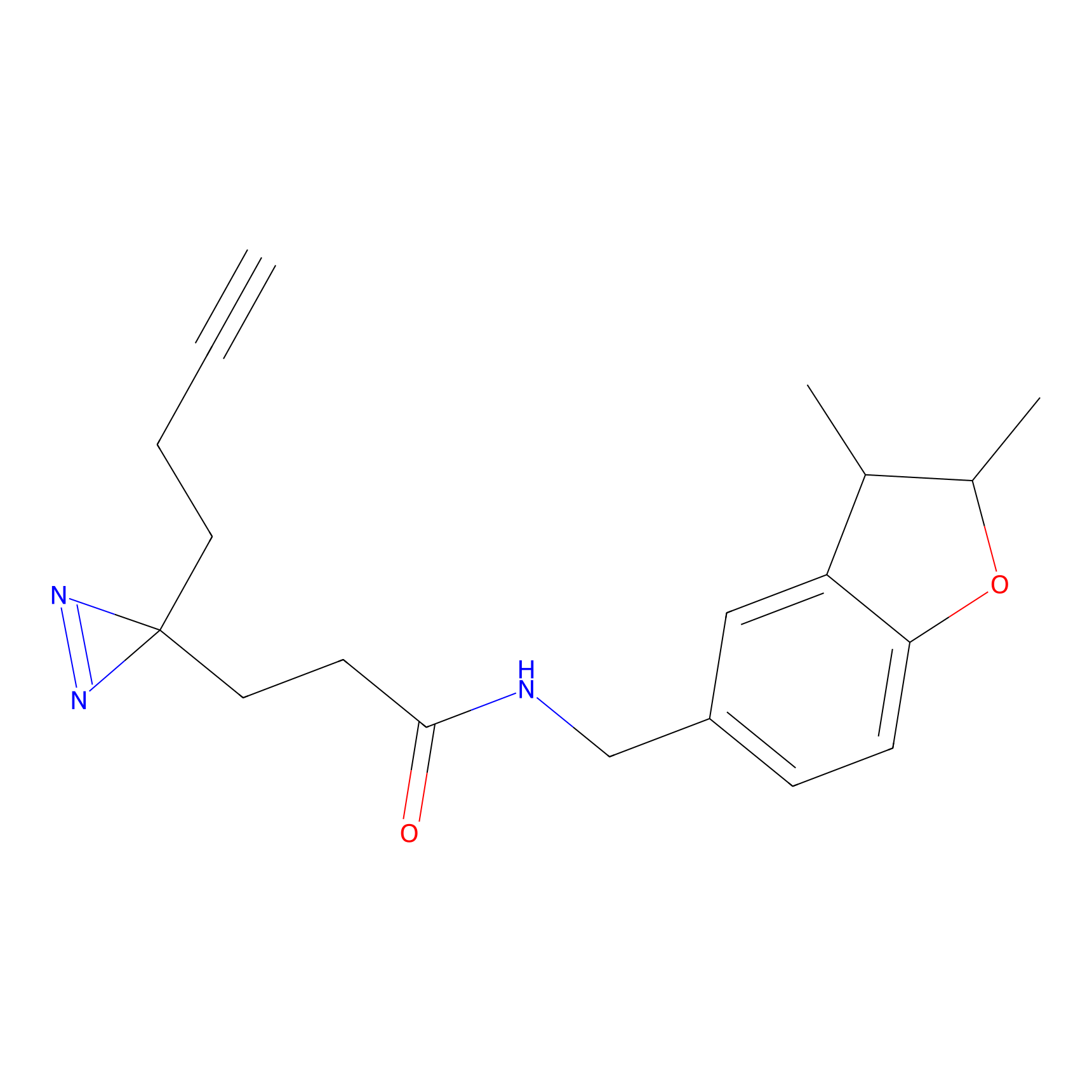
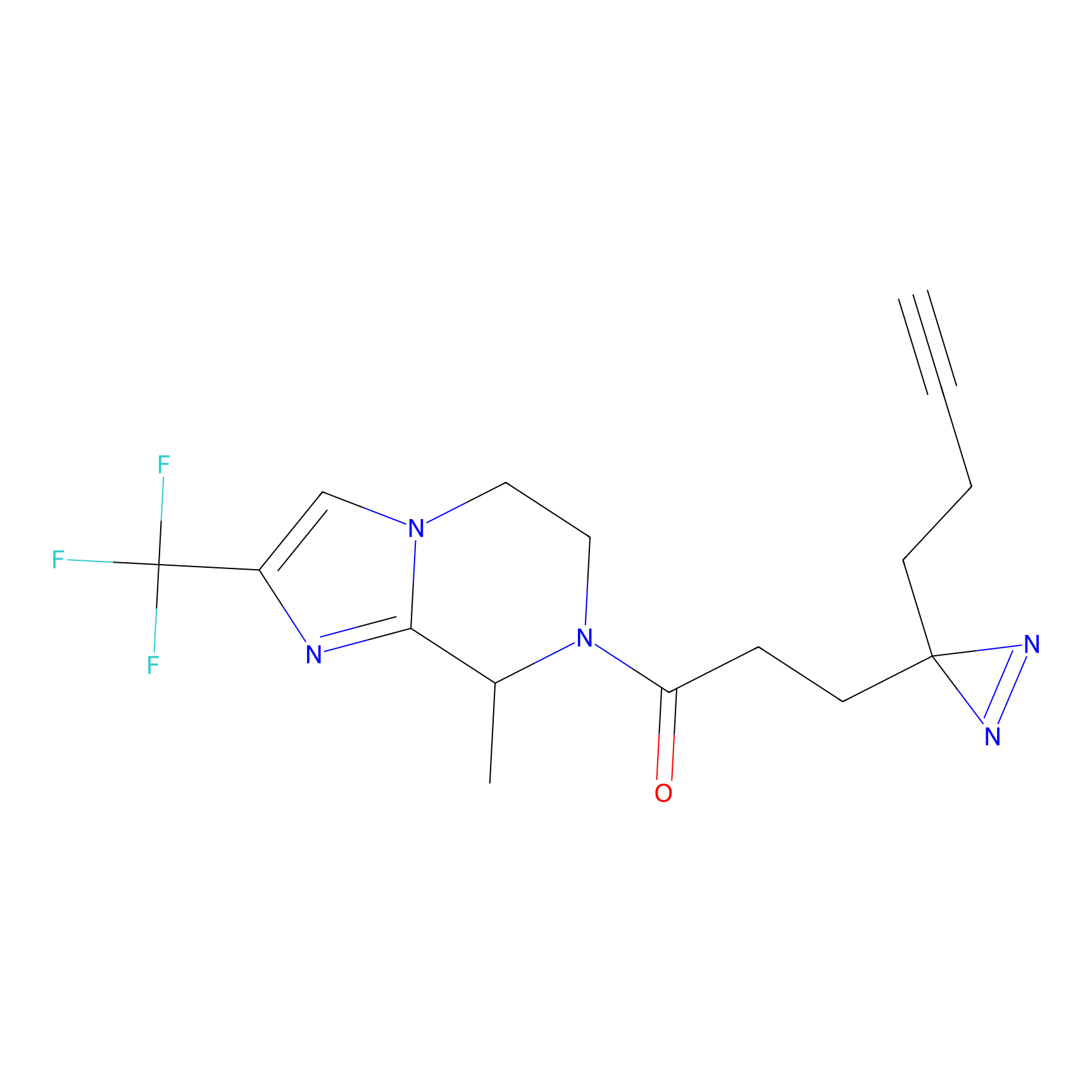
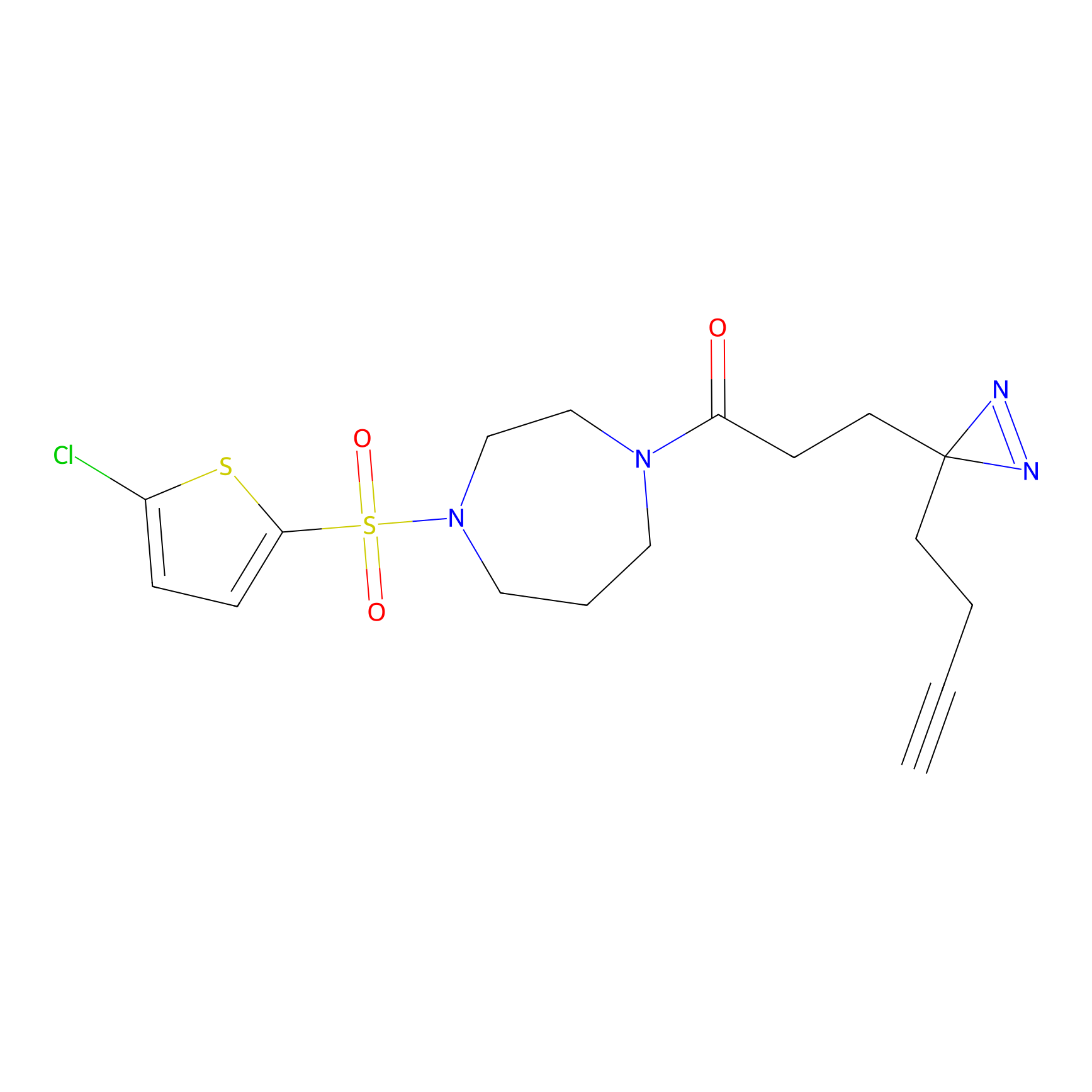
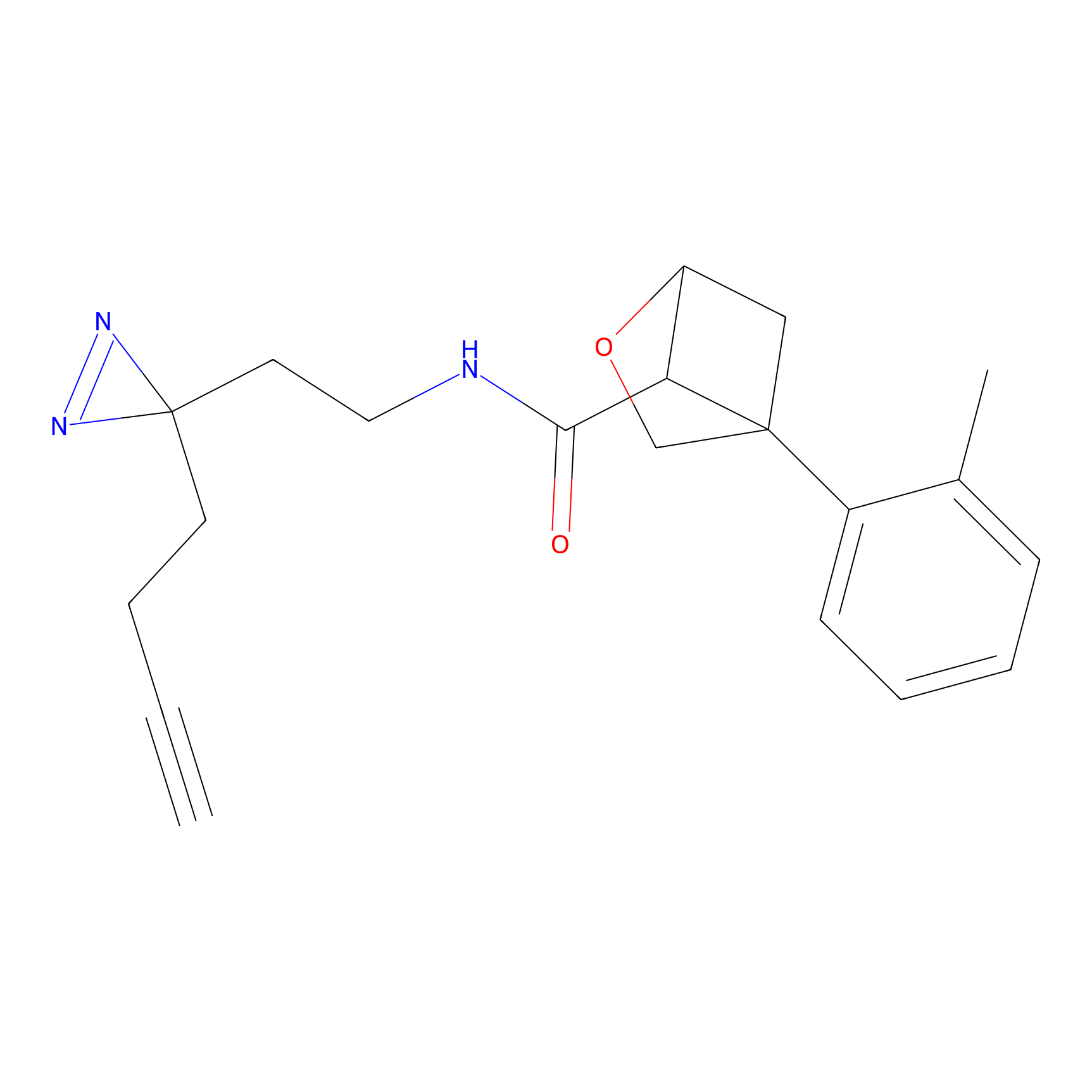
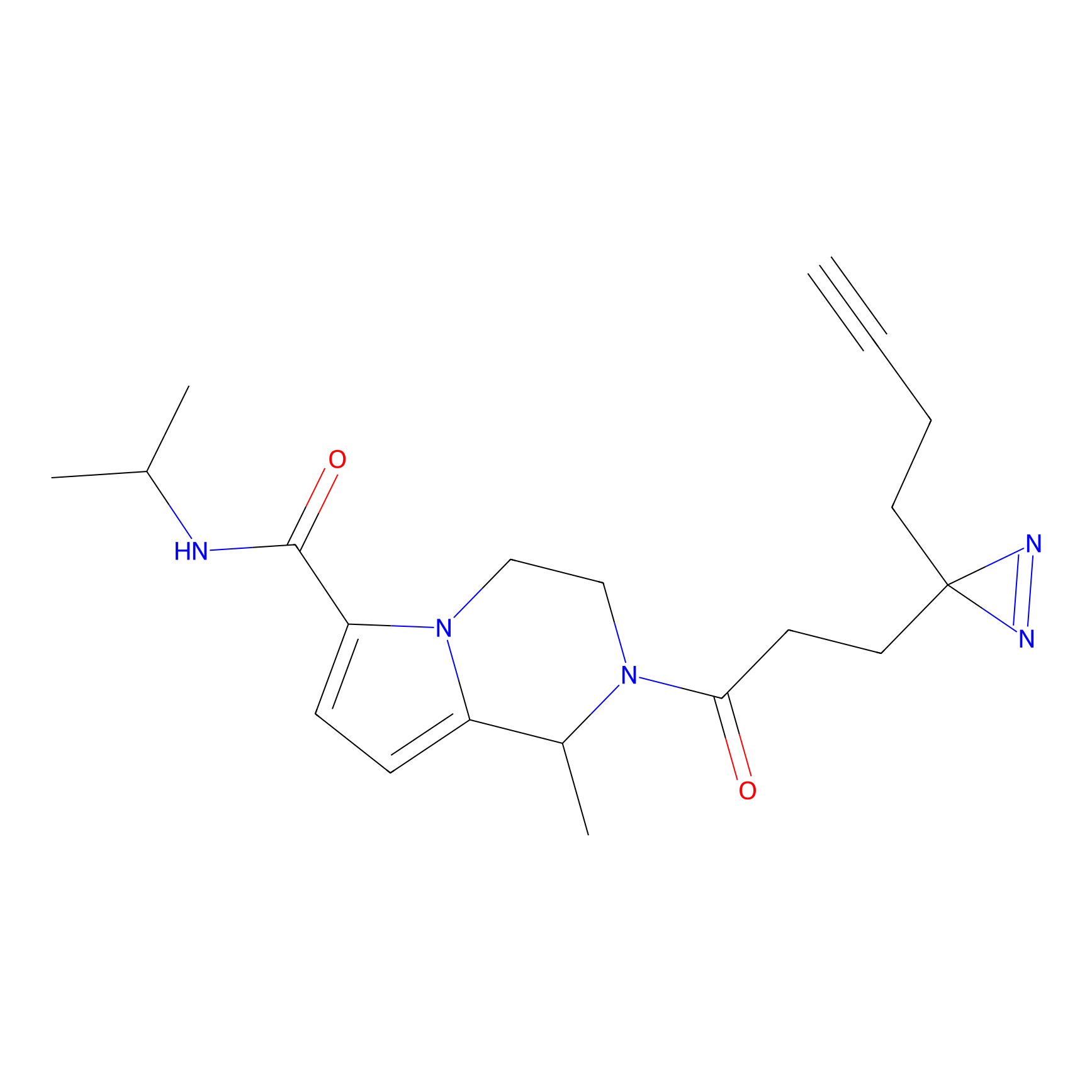
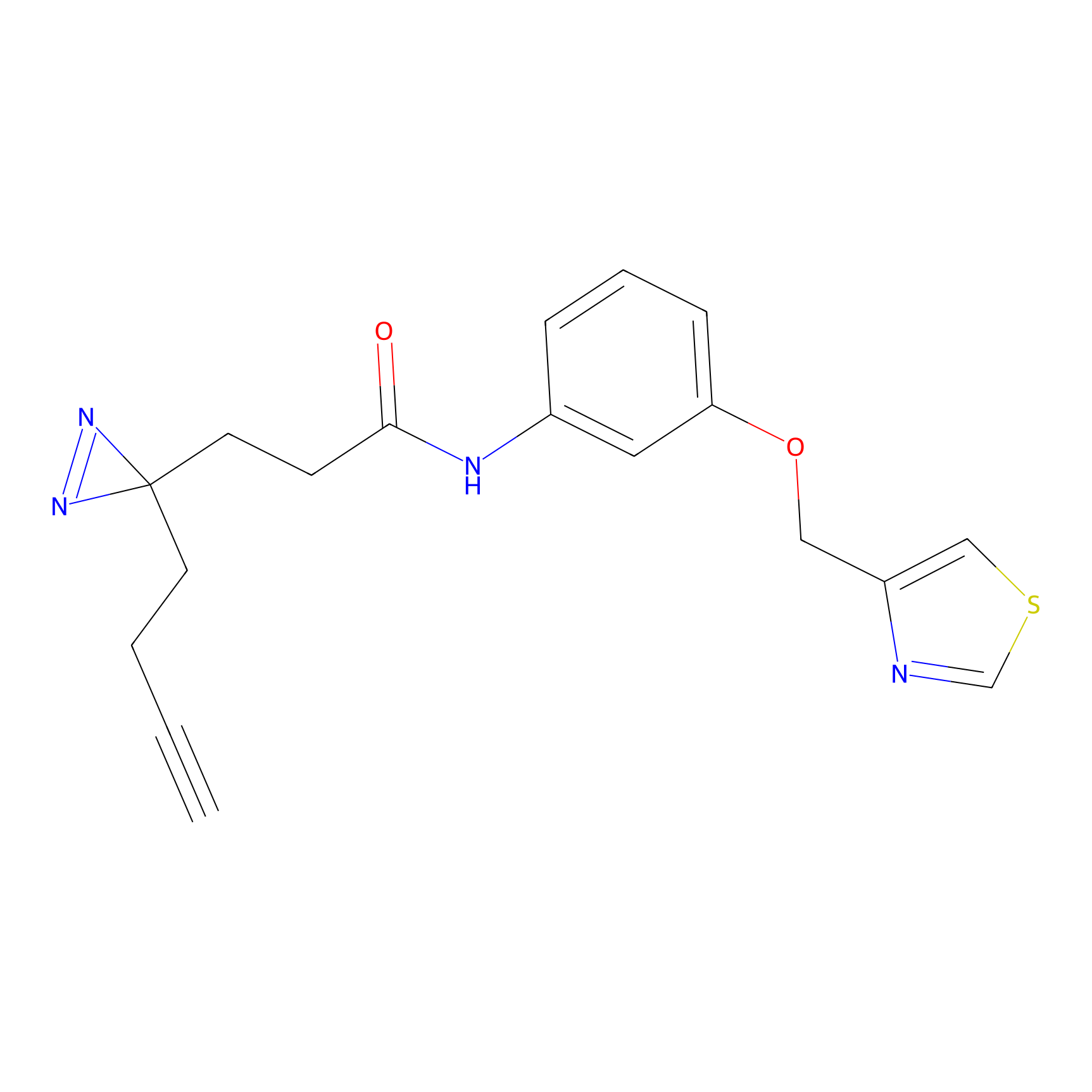
|
TFBX Probe Info |
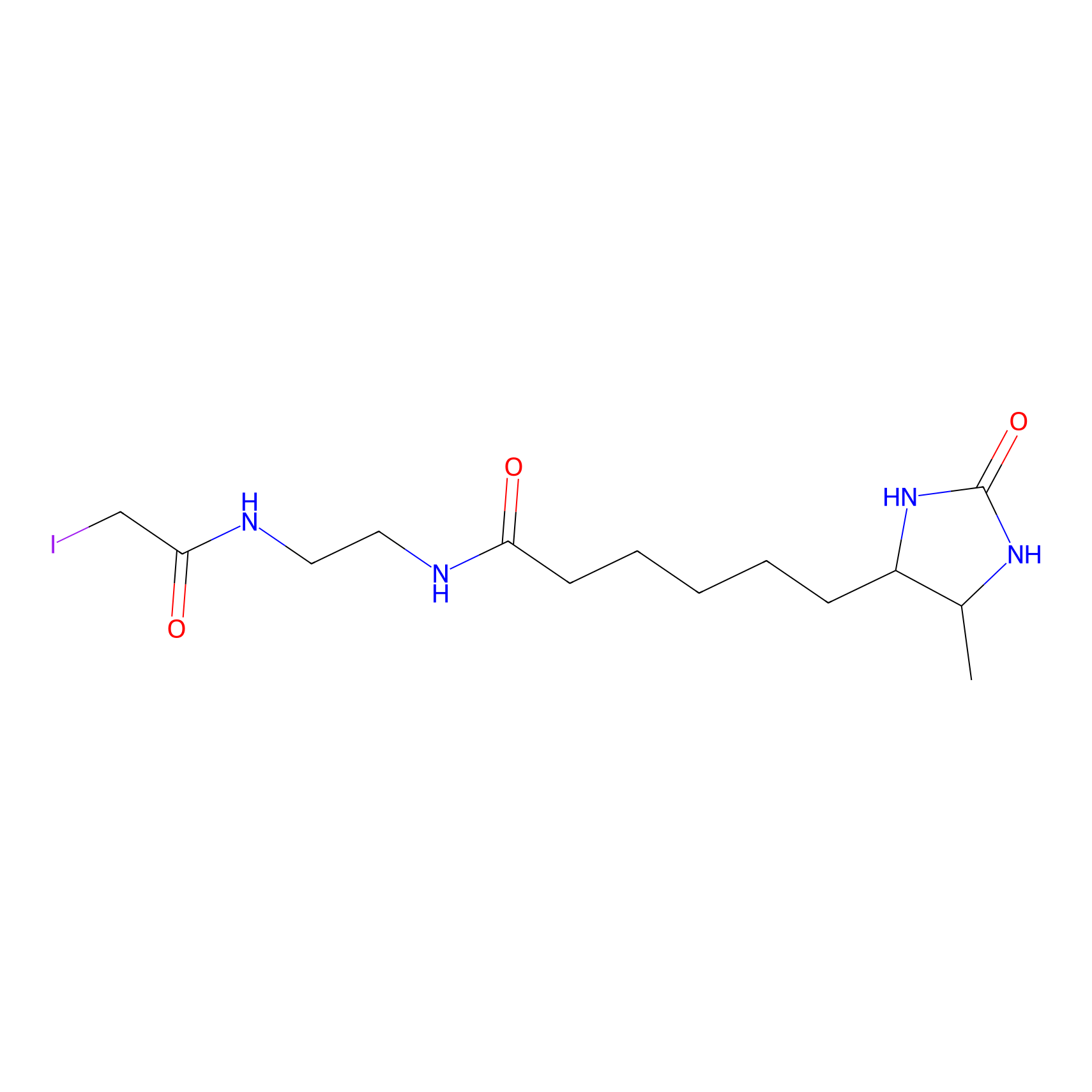
 |
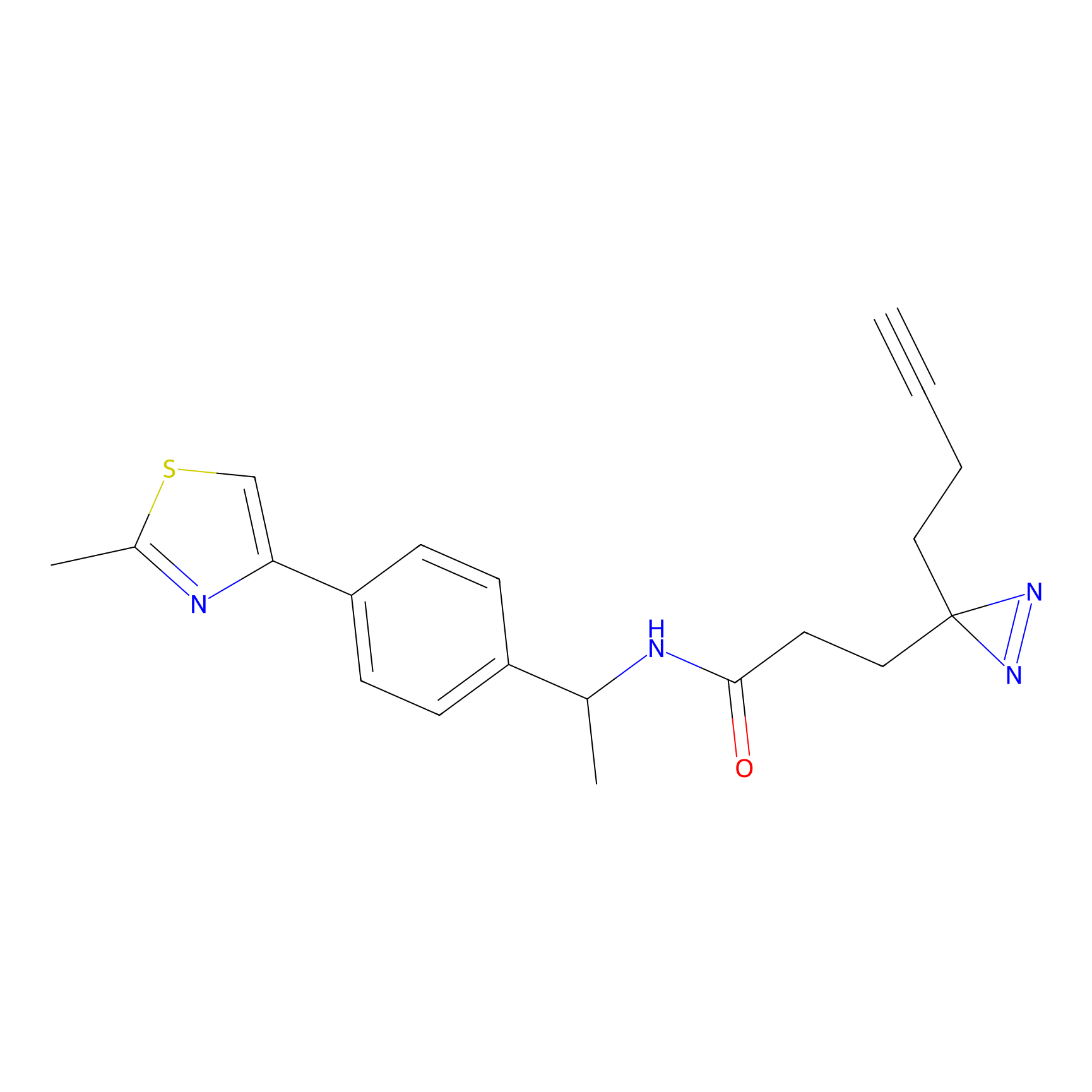
N.A. | LDD0027 | [3] | |
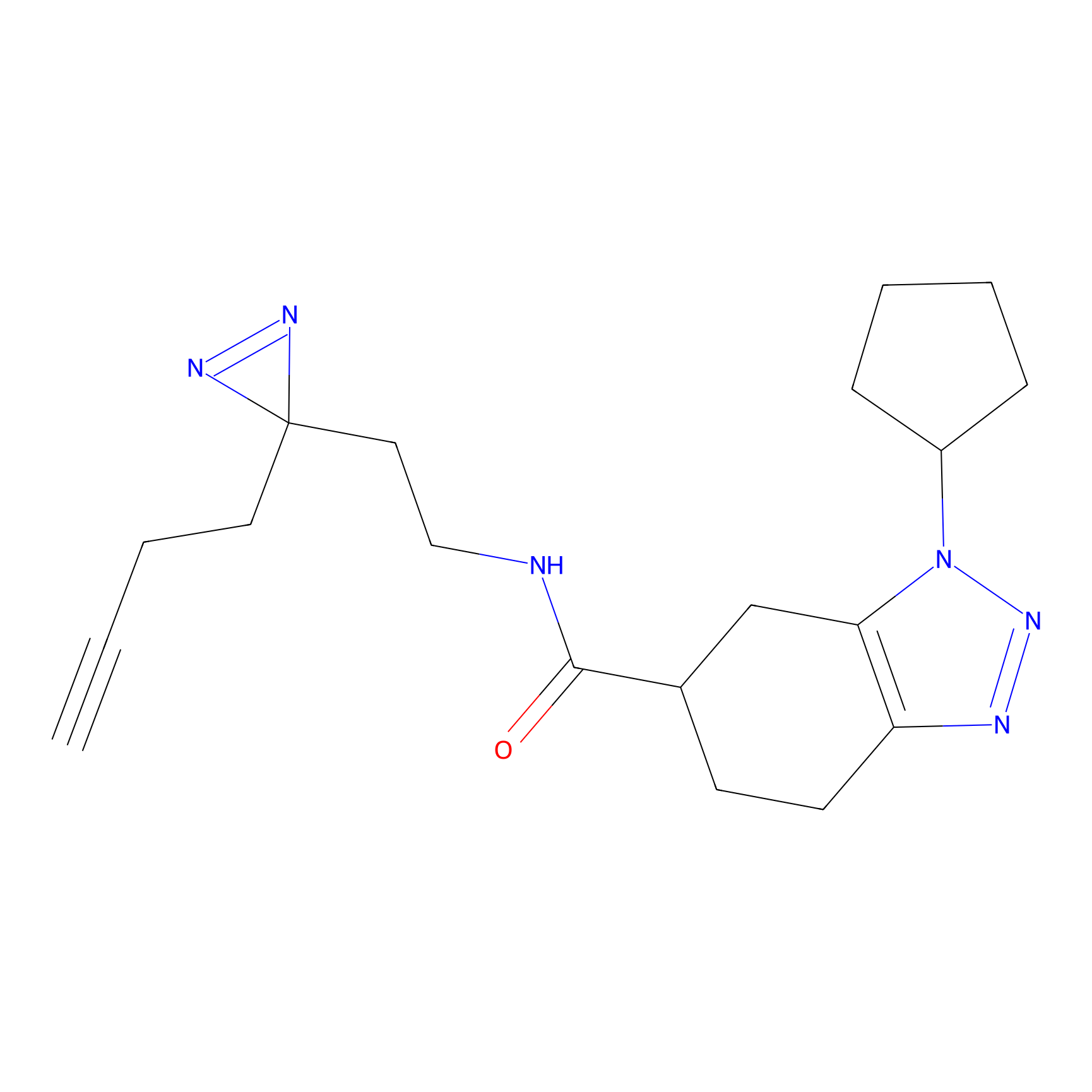
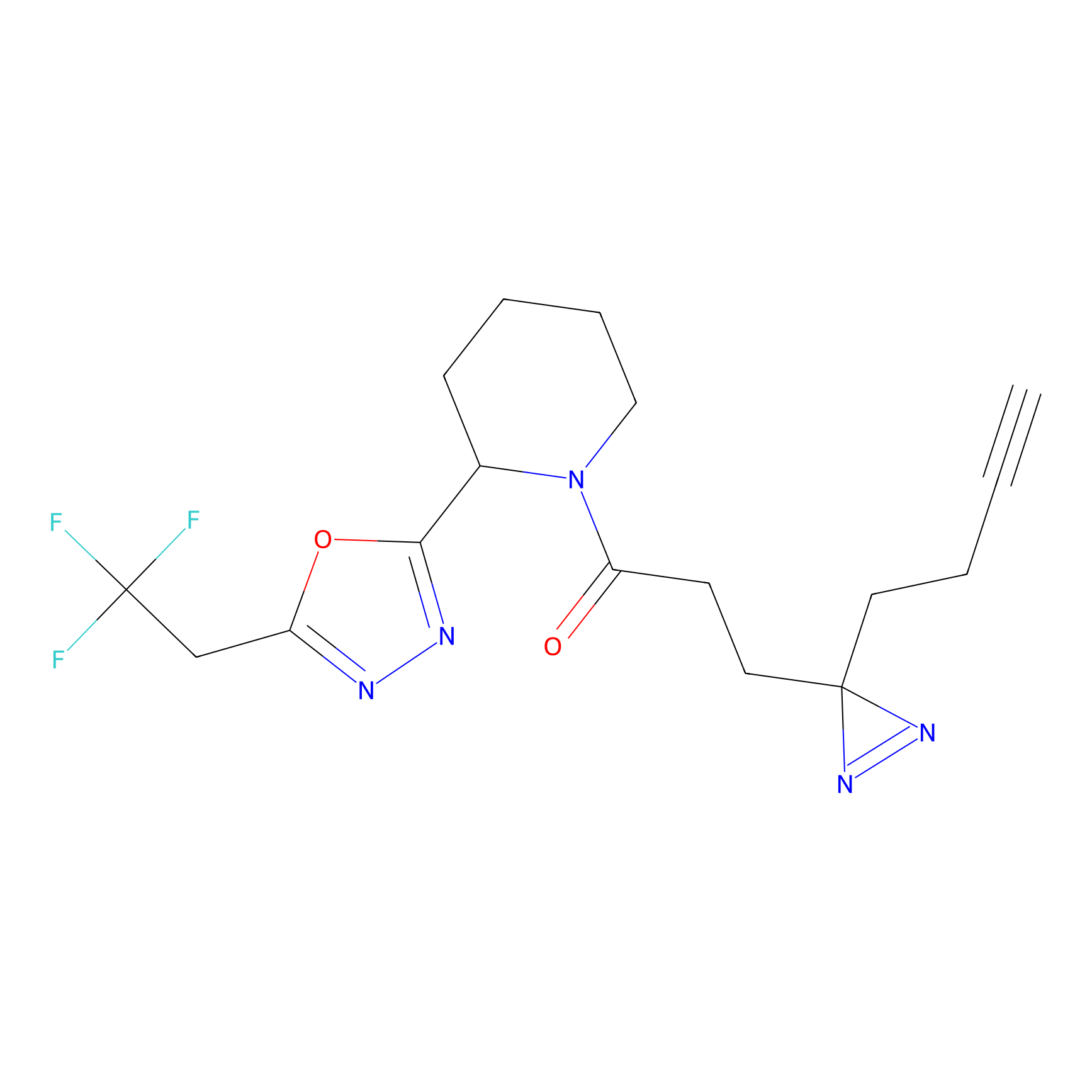
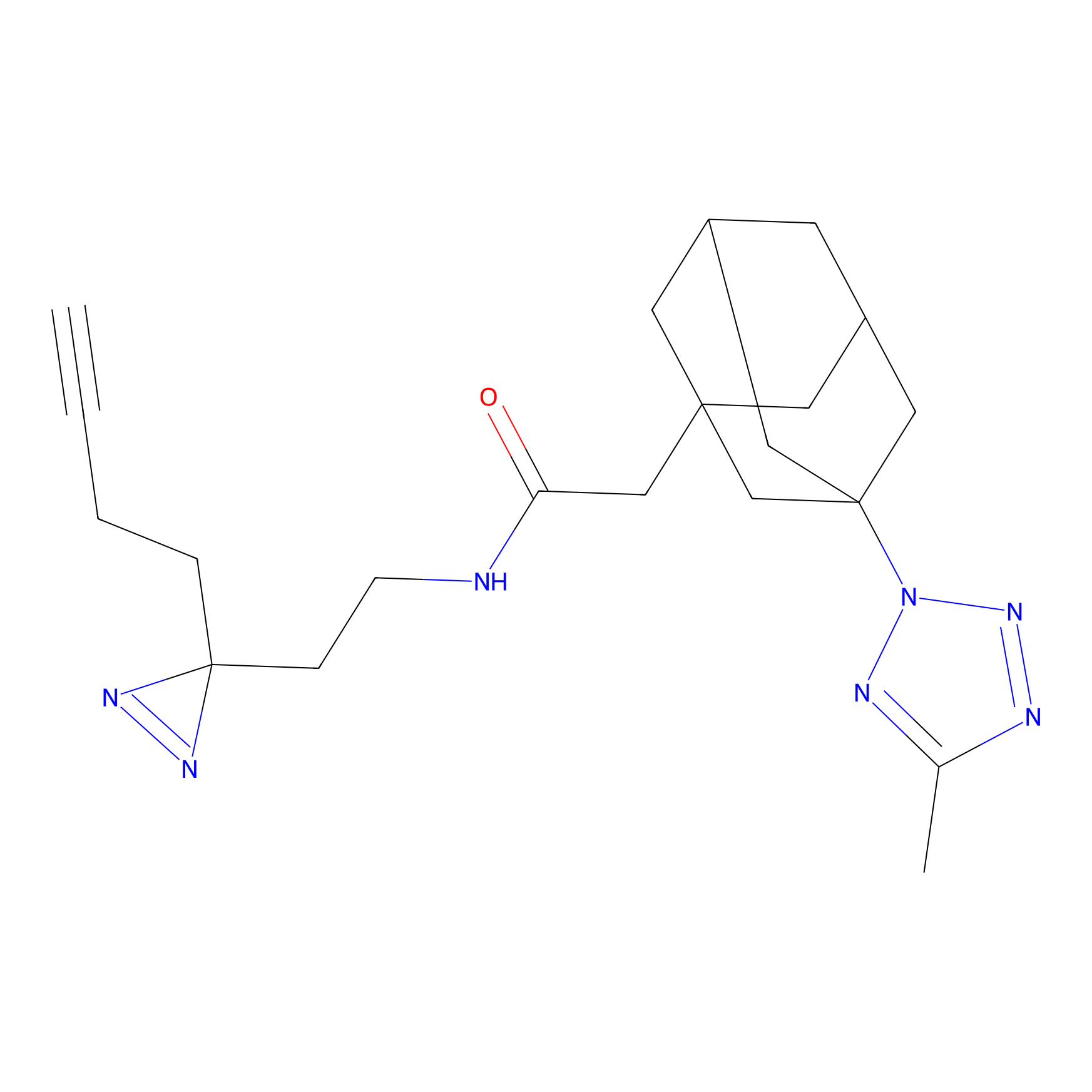
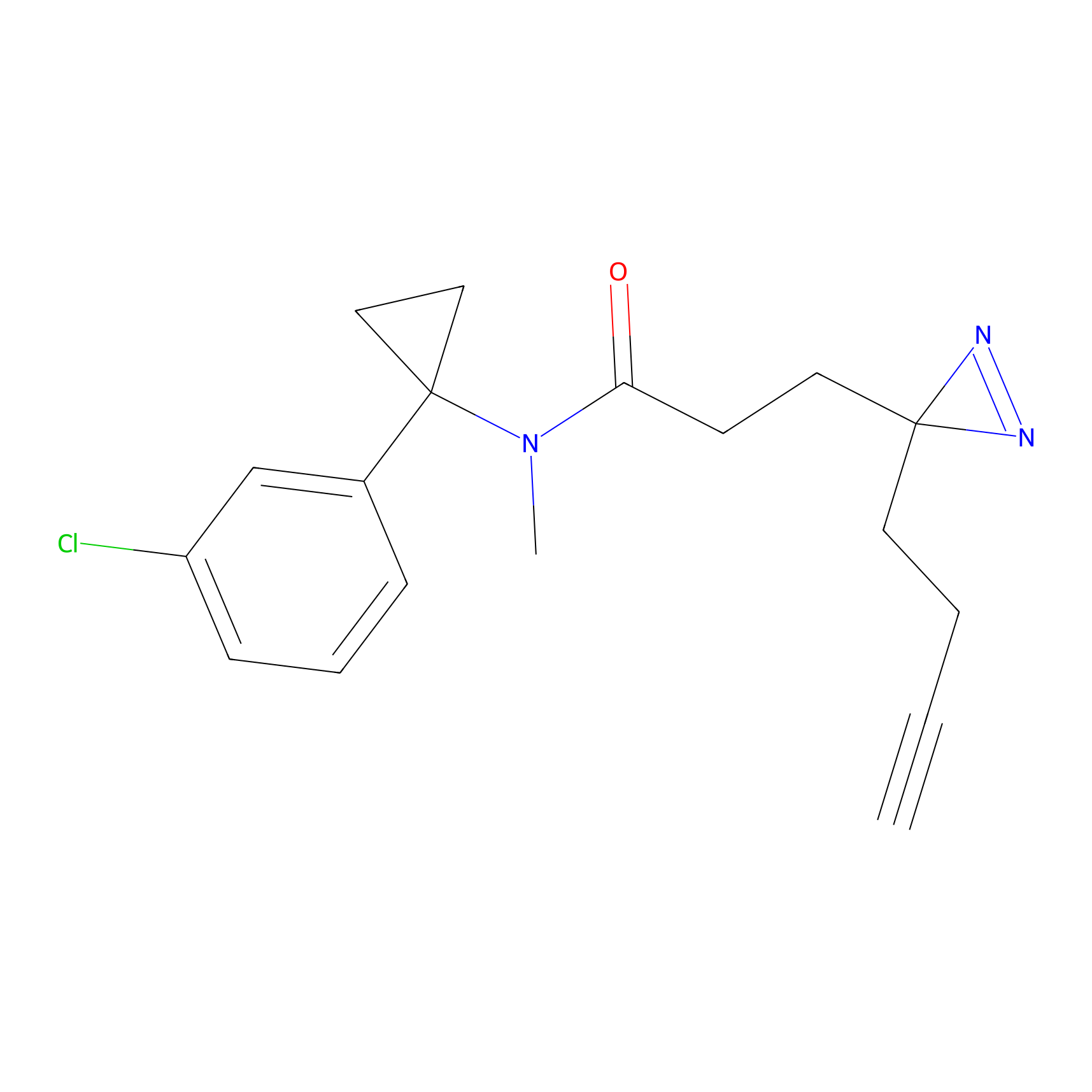
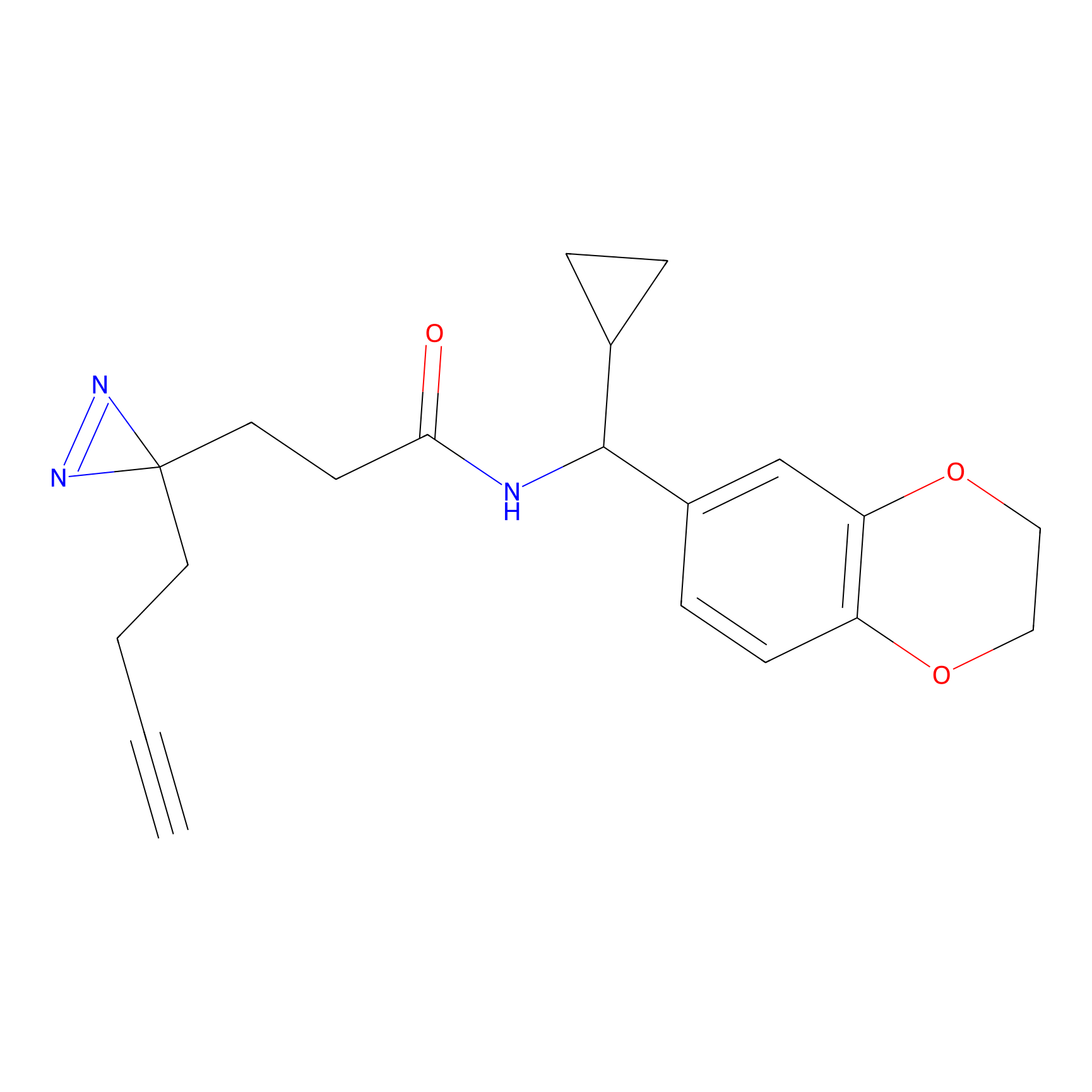
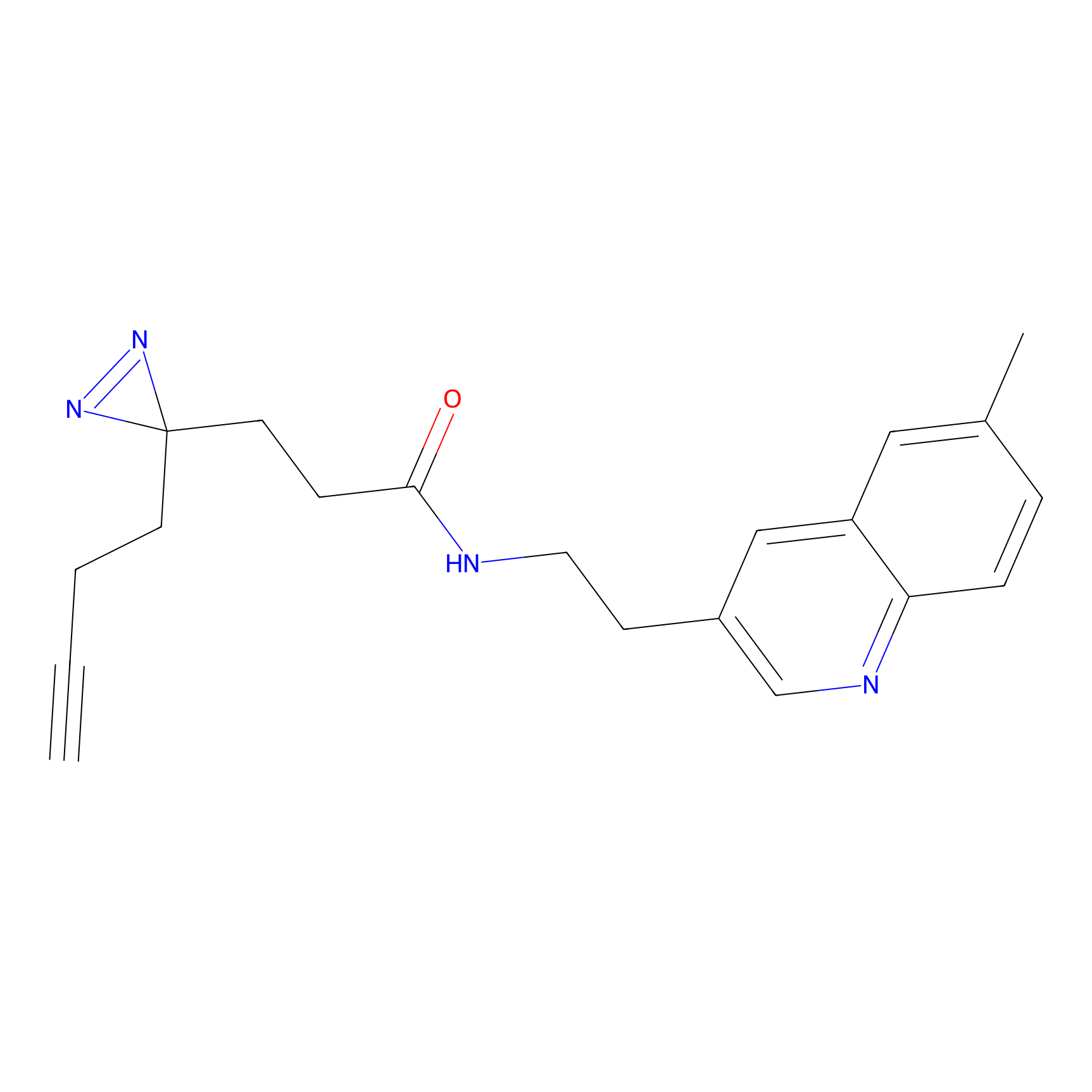
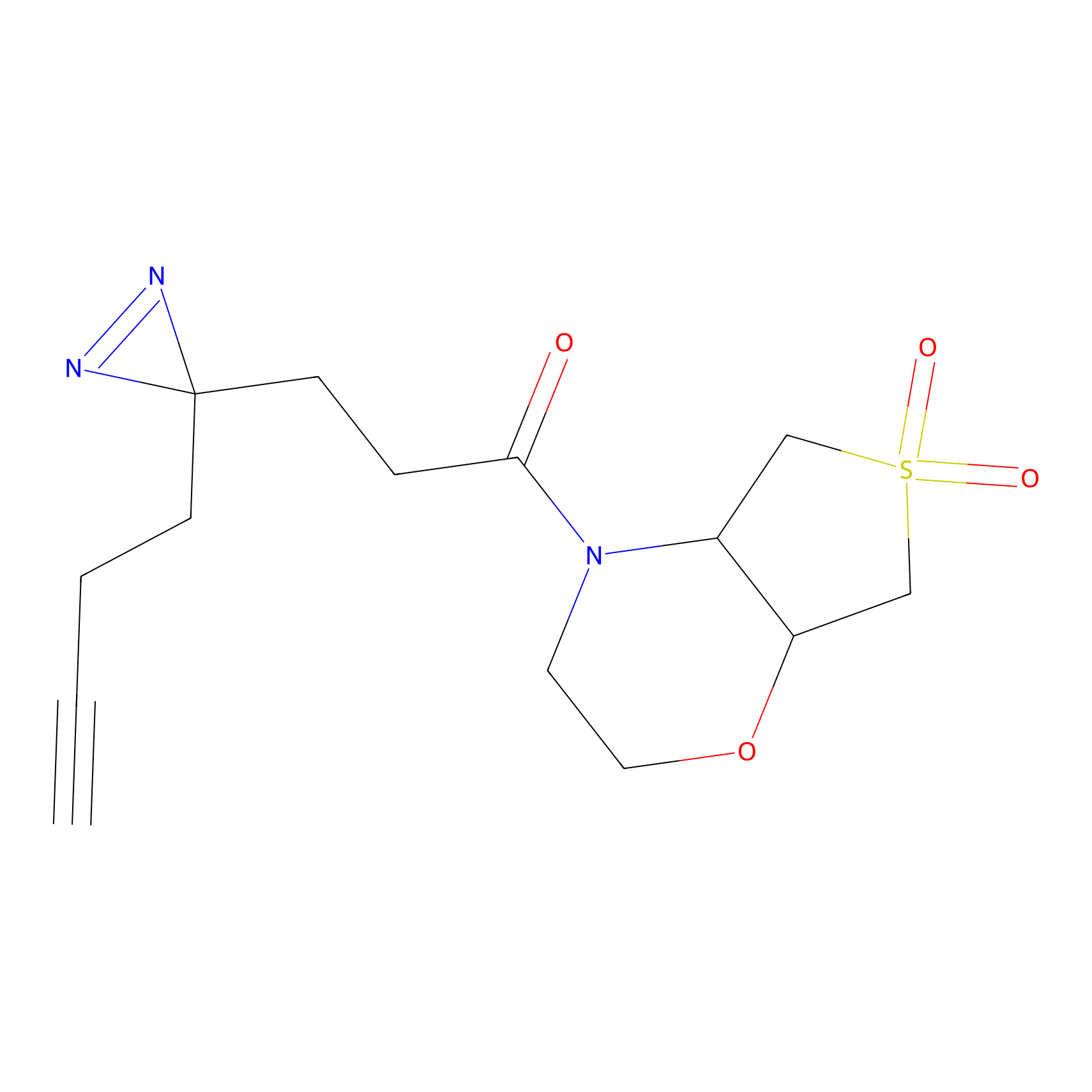
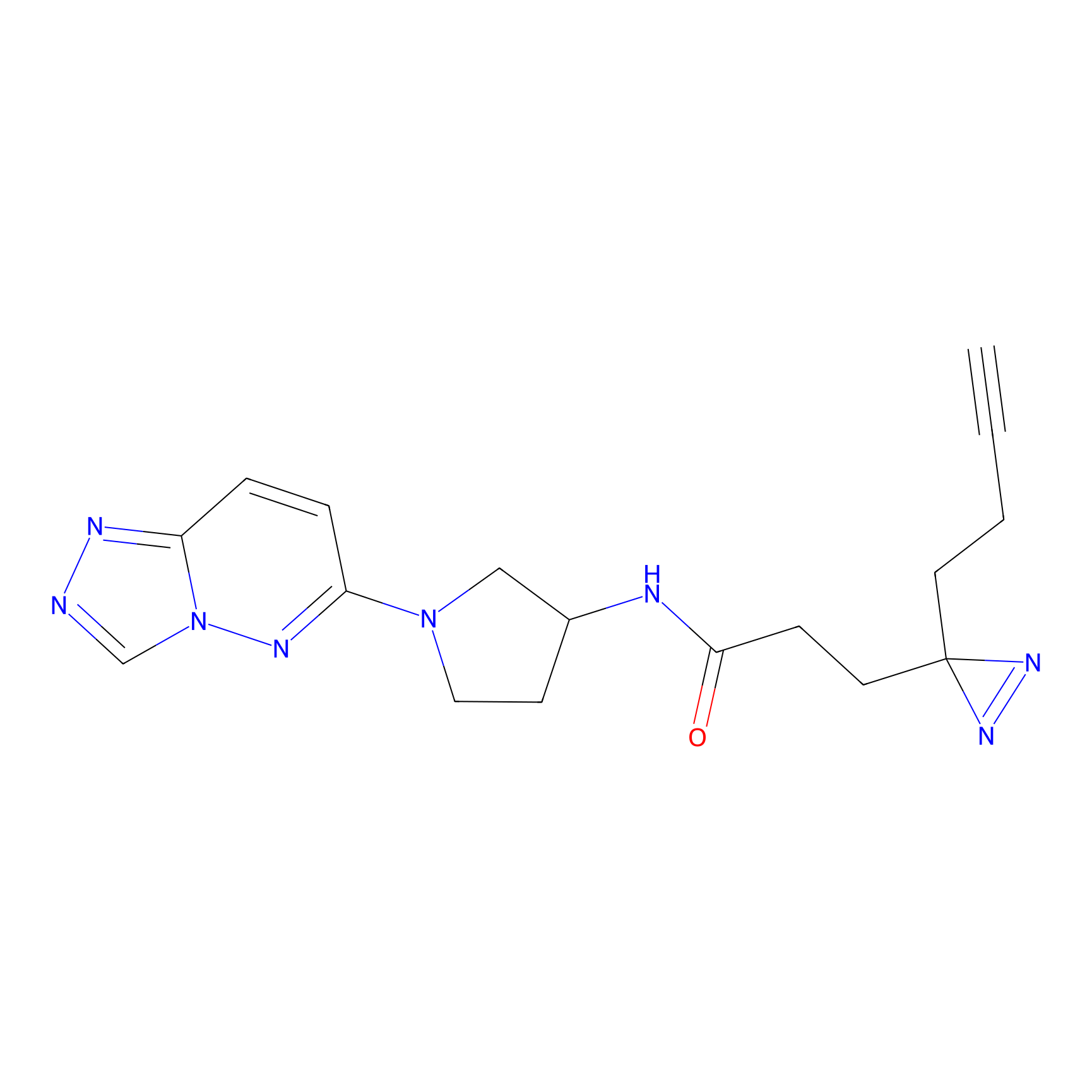
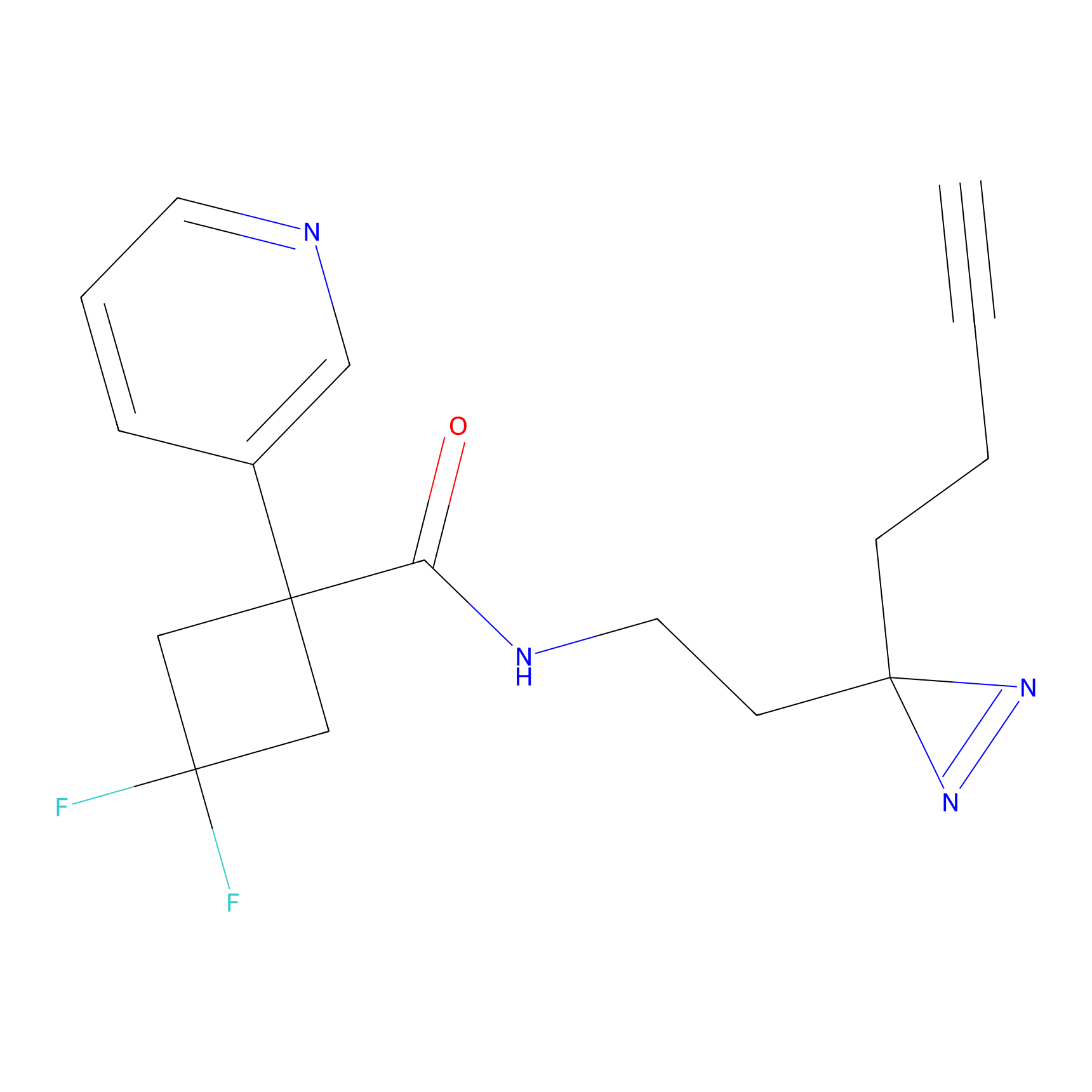
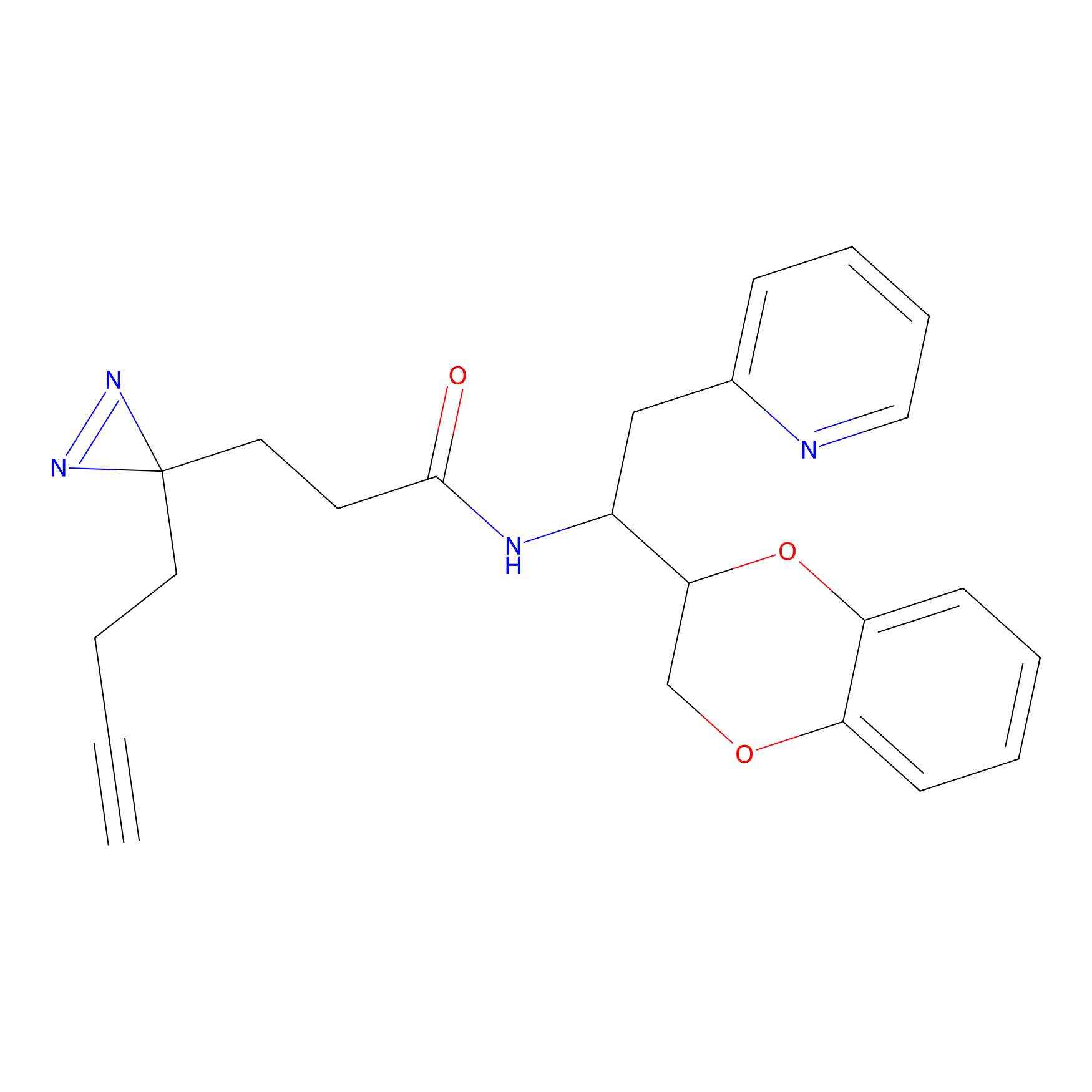
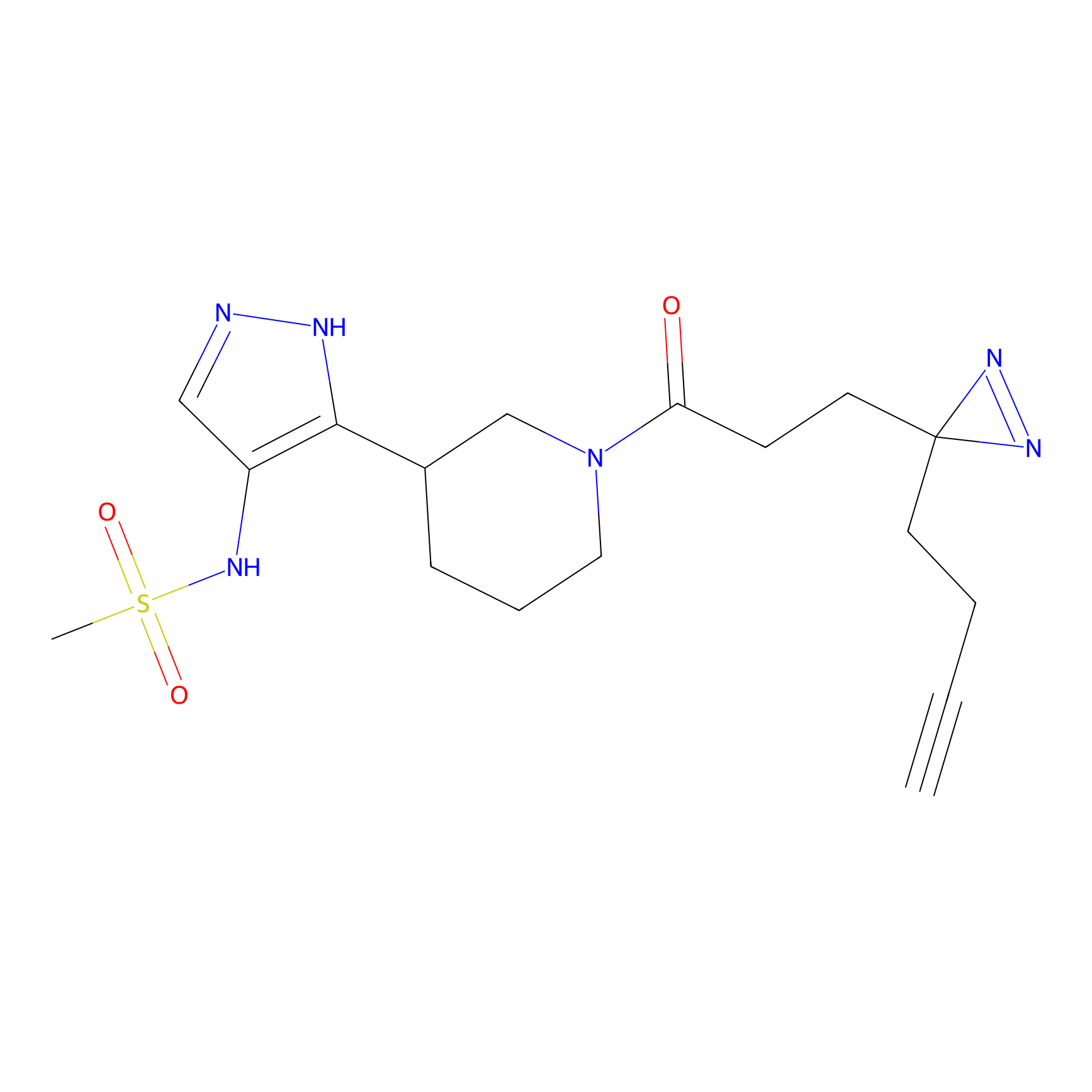
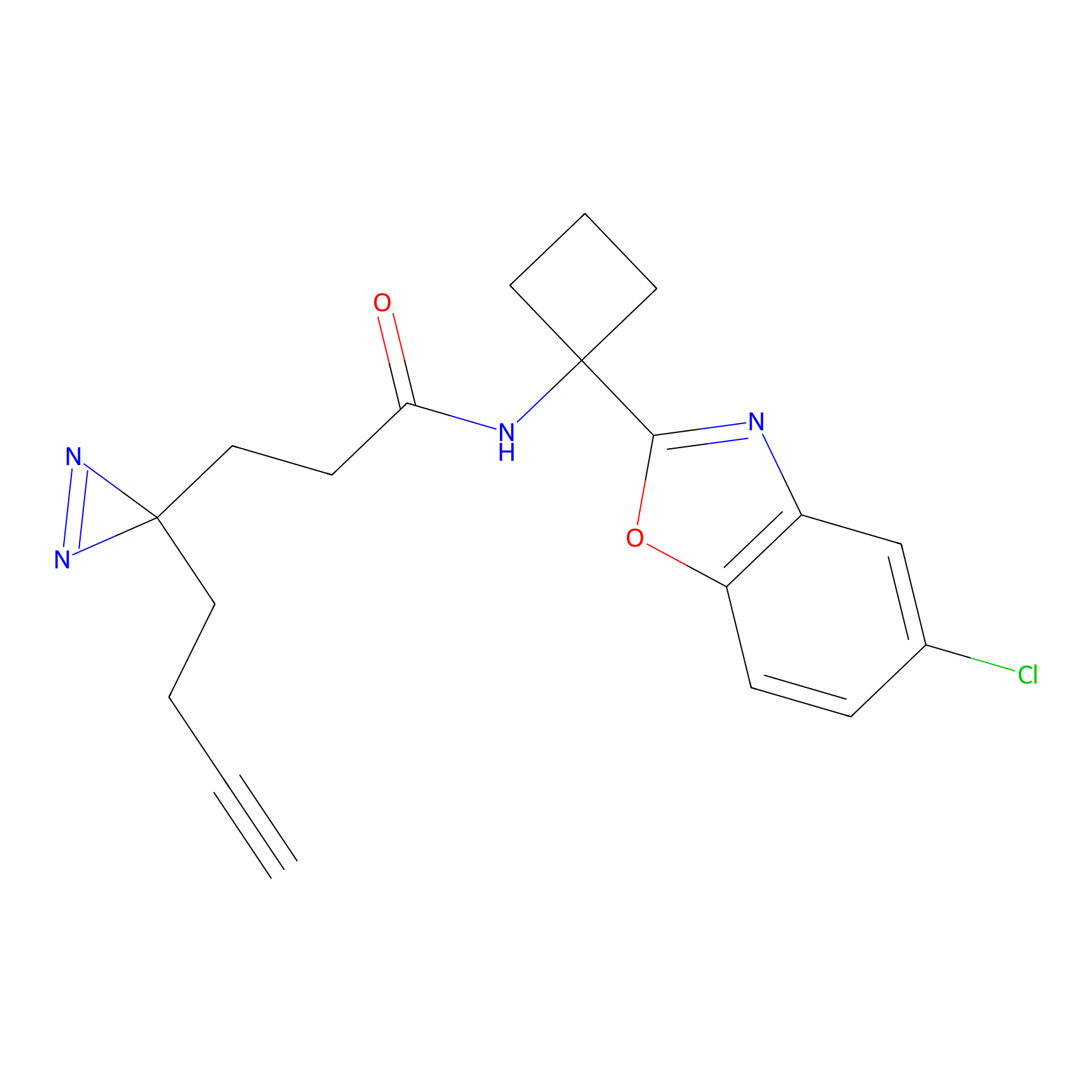
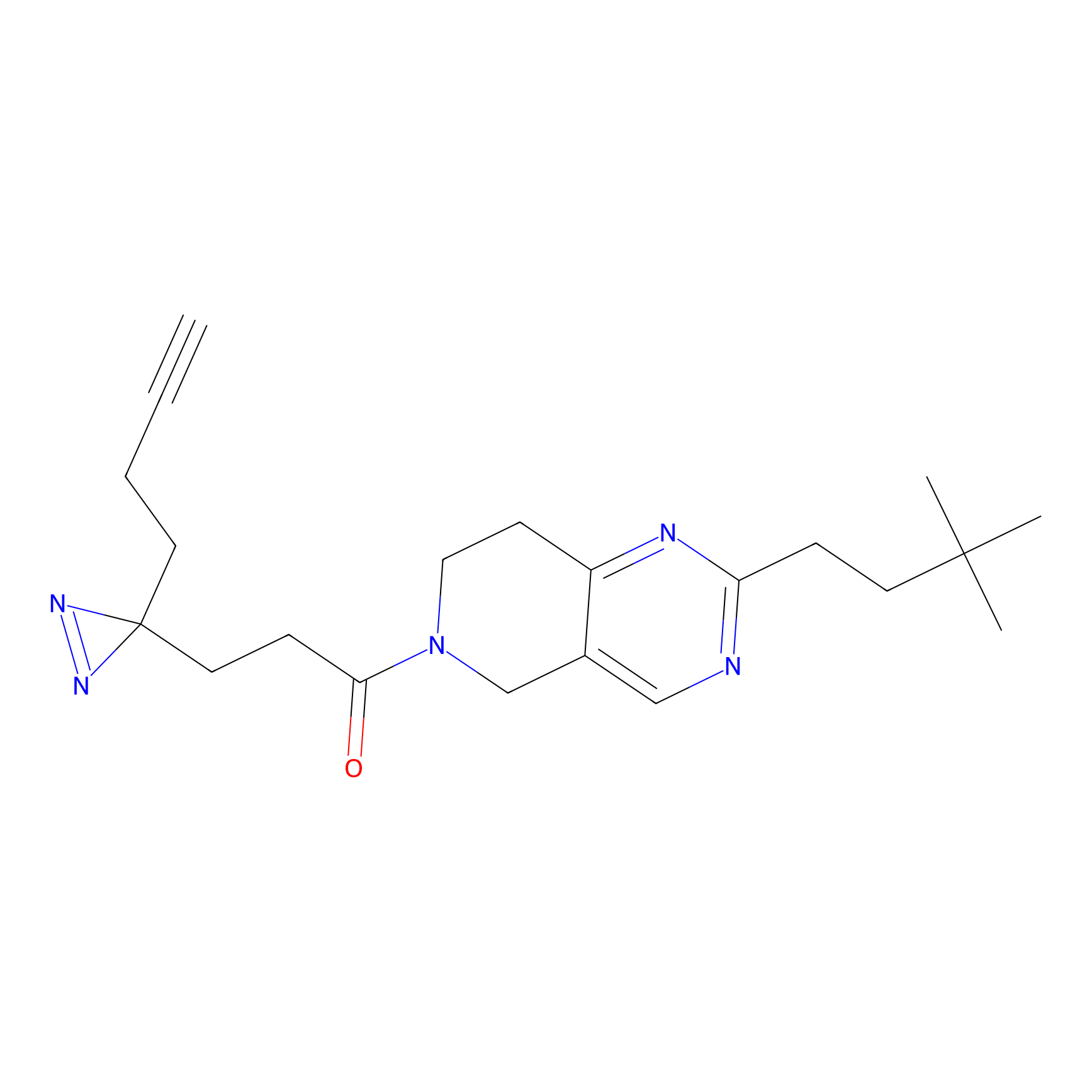
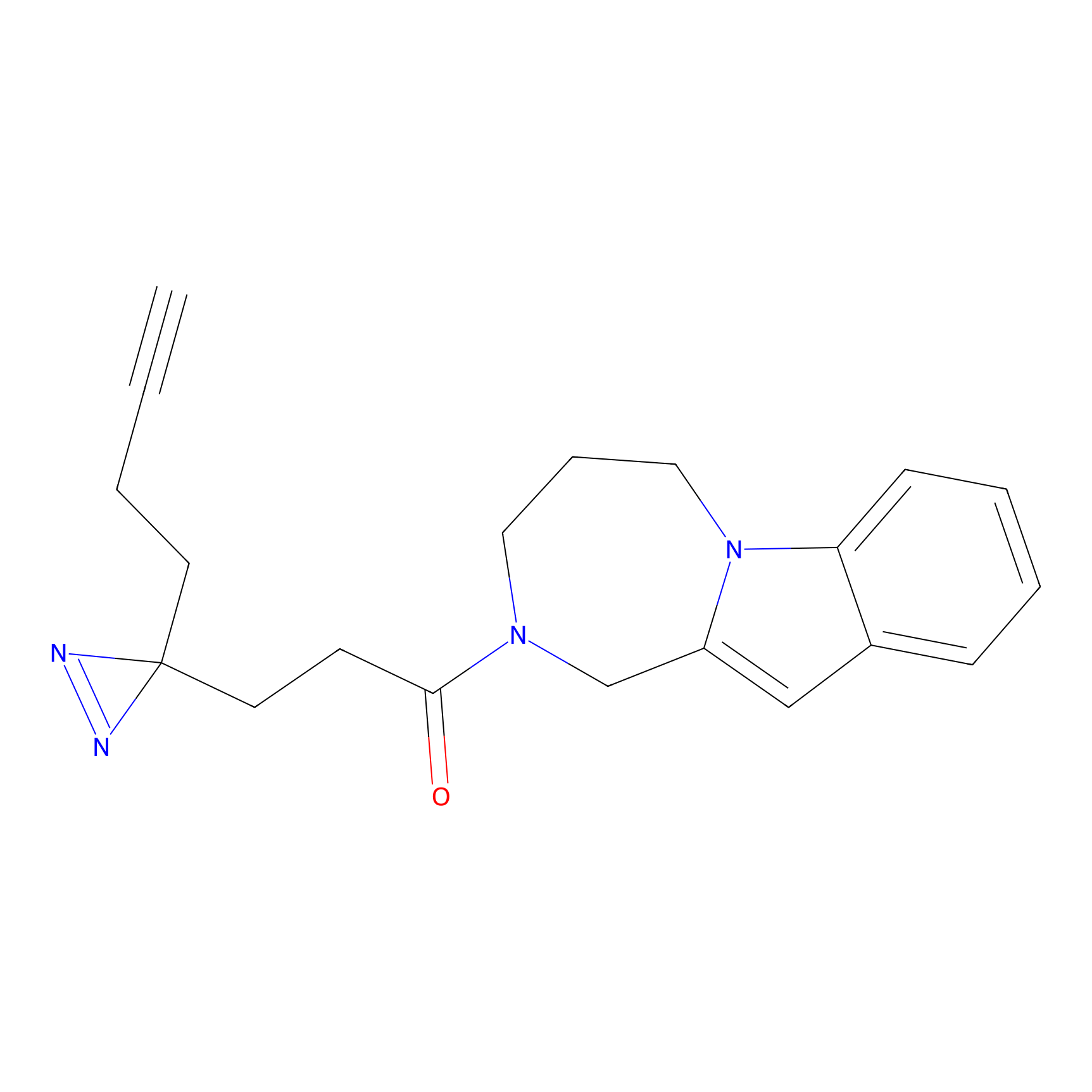
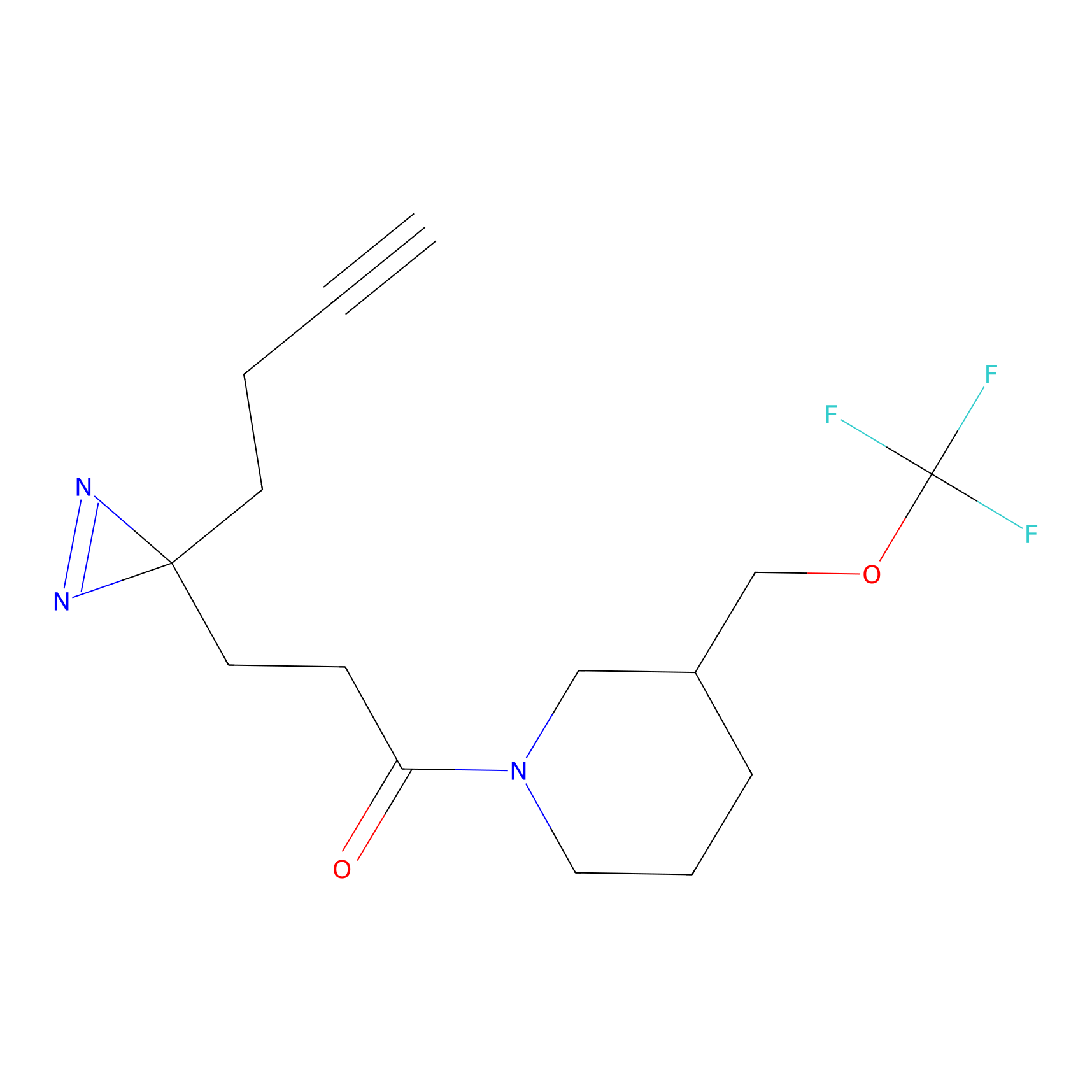
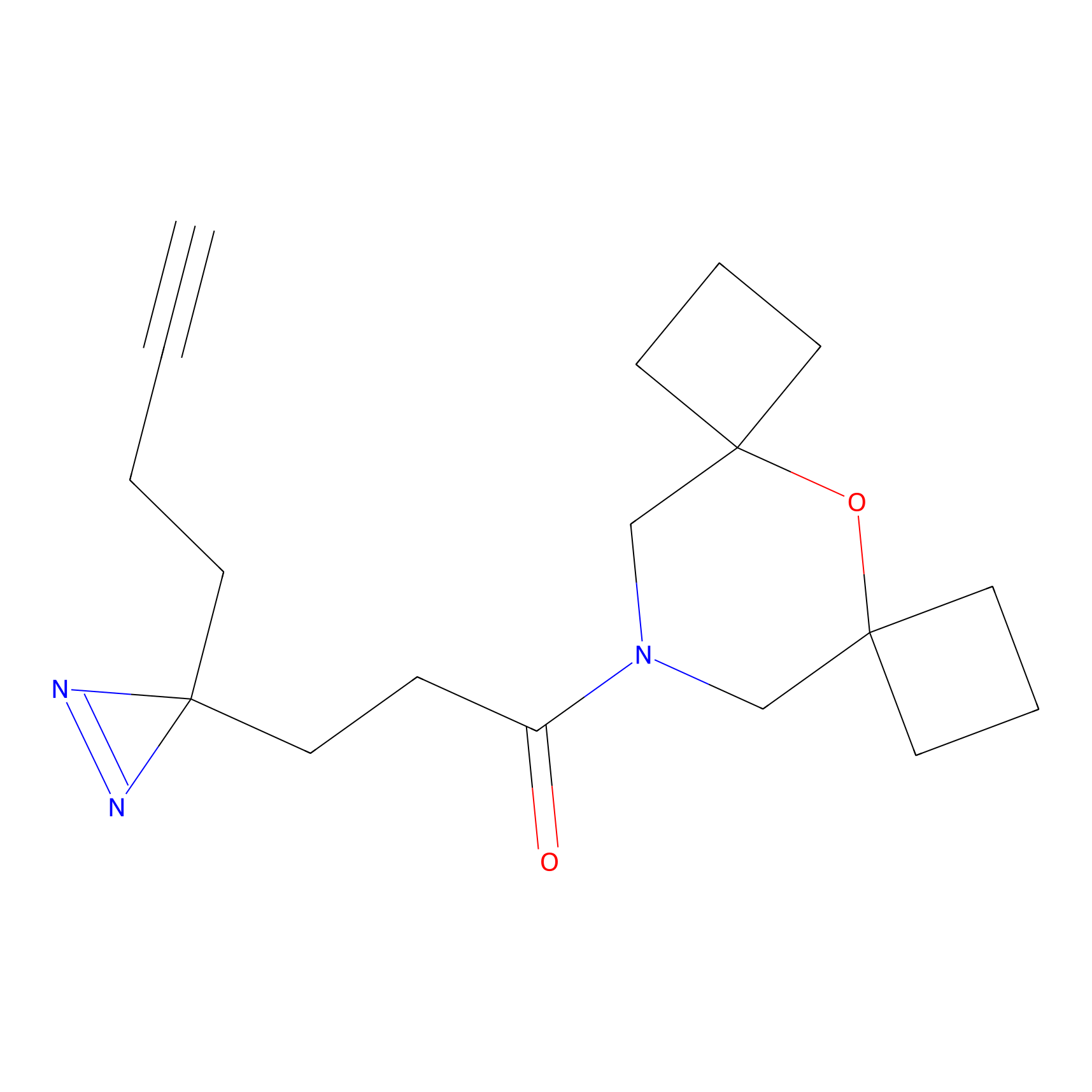
|
IPM Probe Info |
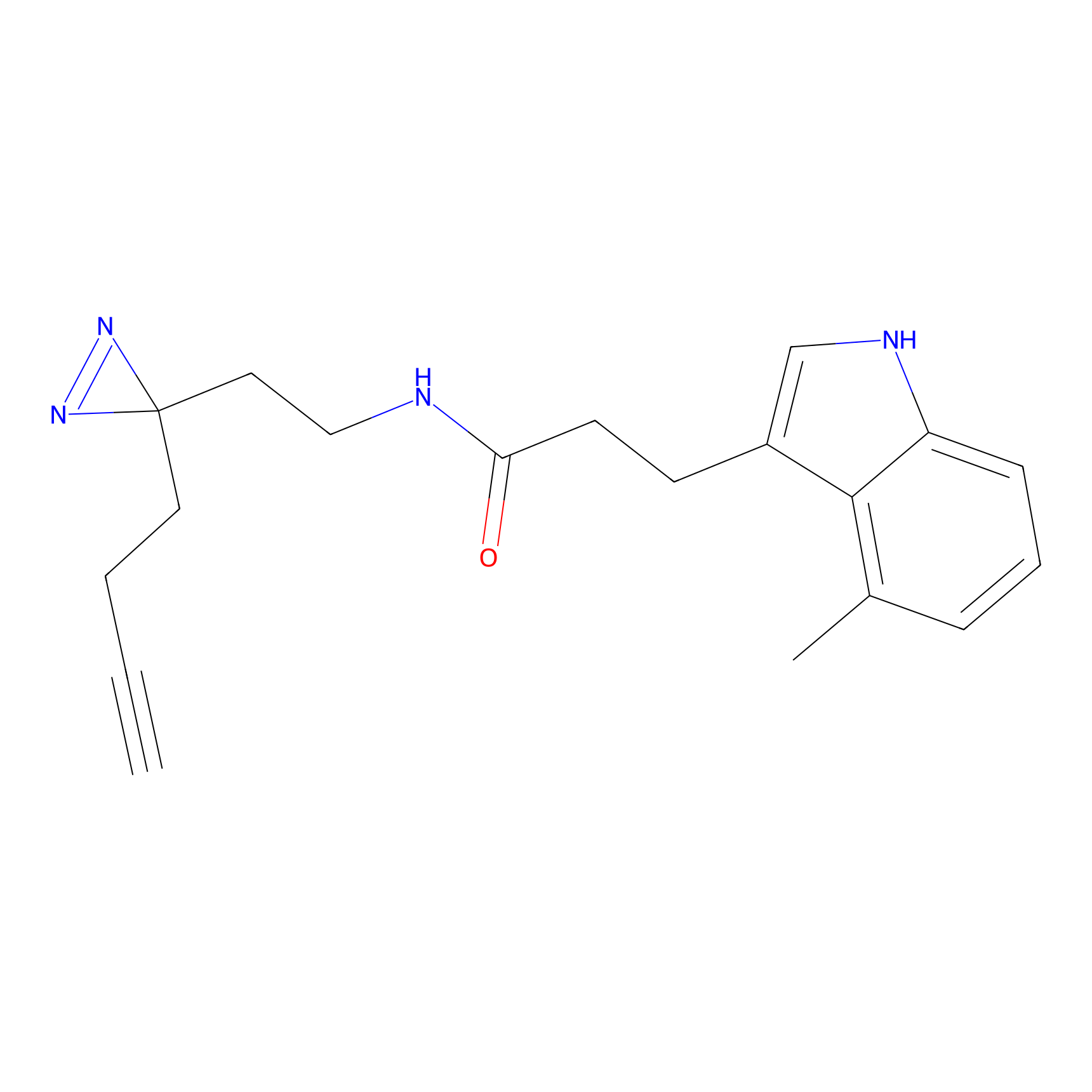
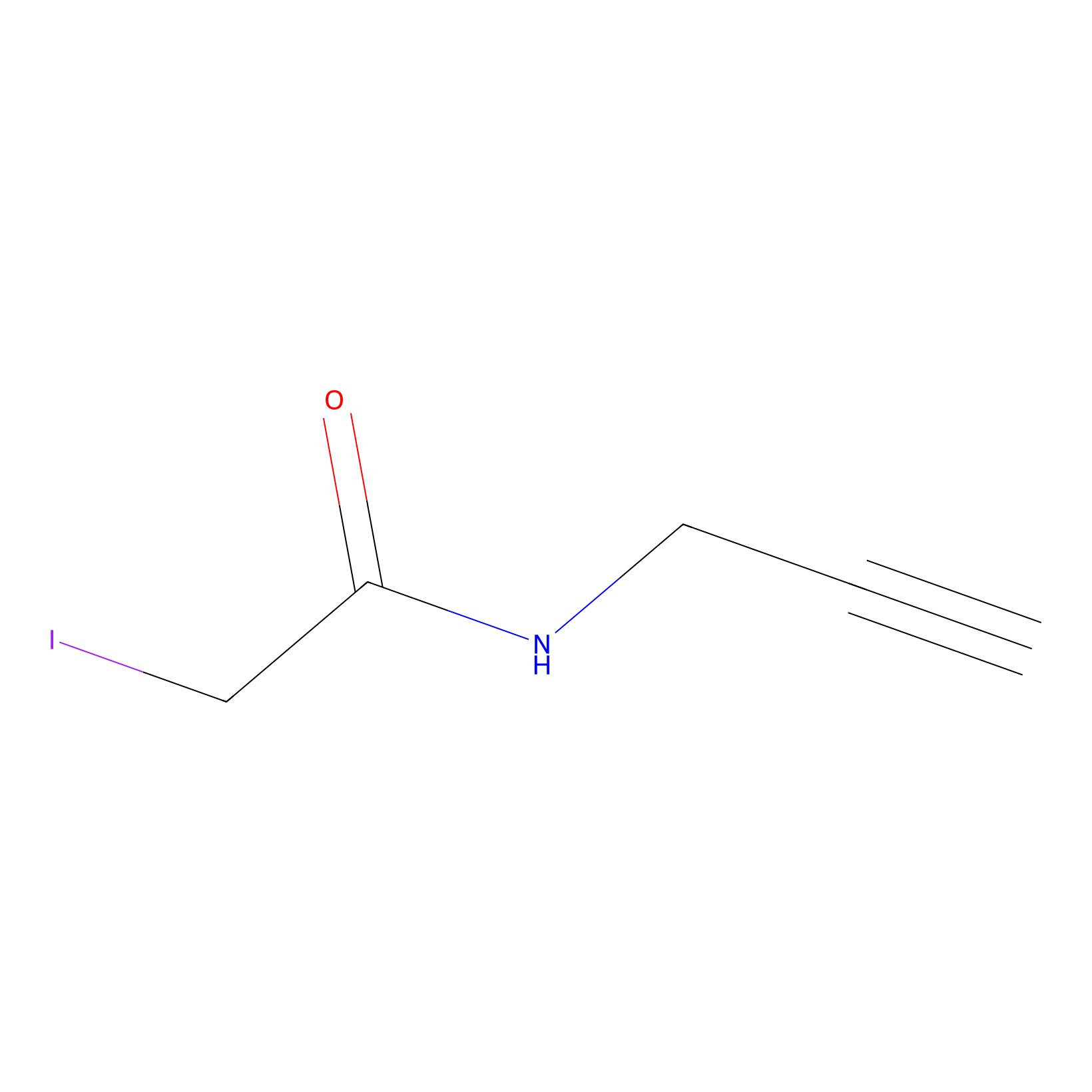 |
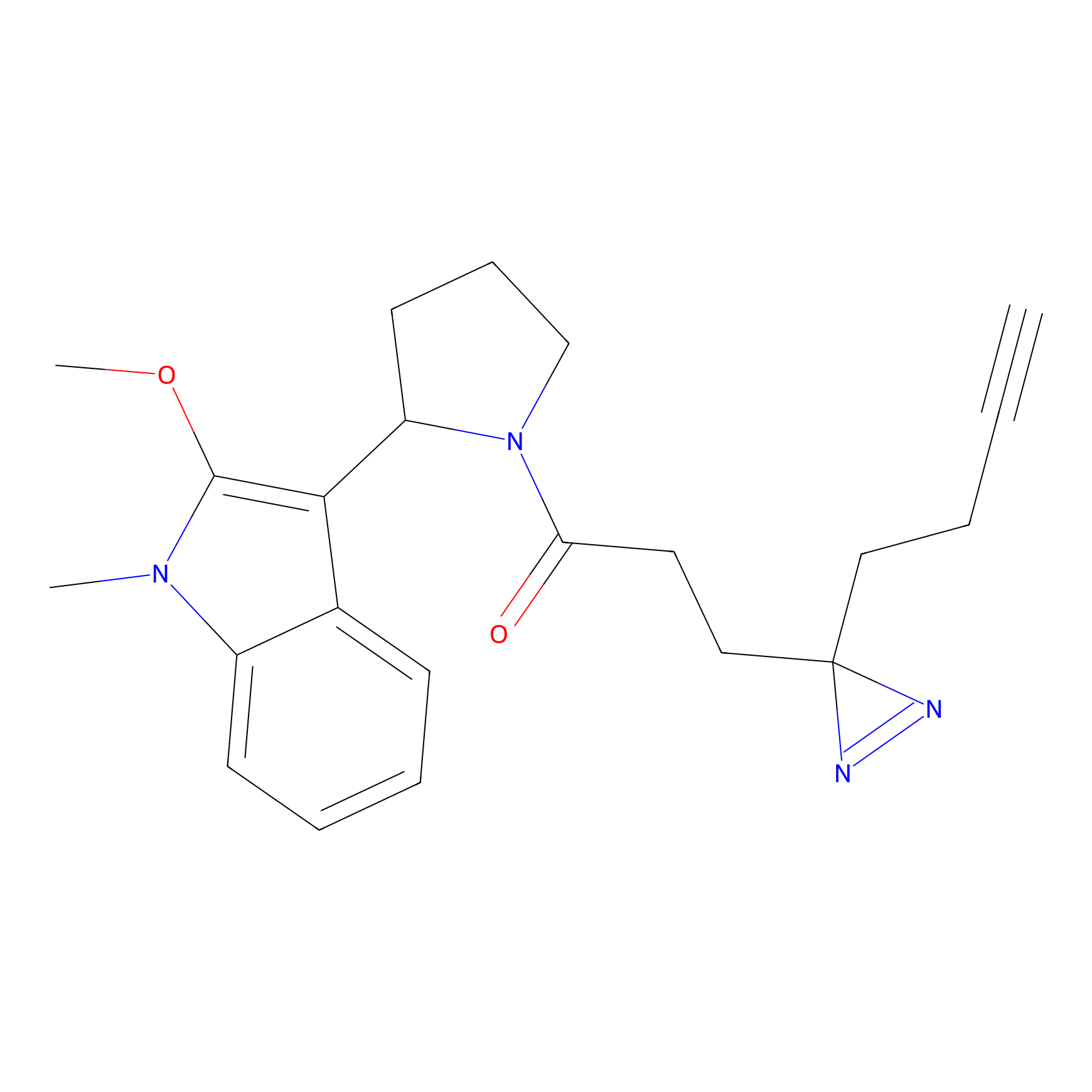
N.A. | LDD2156 | [4] | |
PAL-AfBPP Probe
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0281 | AC21 | HEK-293T | C296(0.89) | LDD1520 | [2] |
| LDCM0284 | AC24 | HEK-293T | C296(1.55) | LDD1523 | [2] |
| LDCM0289 | AC29 | HEK-293T | C296(0.99) | LDD1528 | [2] |
| LDCM0293 | AC32 | HEK-293T | C296(1.25) | LDD1532 | [2] |
| LDCM0298 | AC37 | HEK-293T | C296(0.99) | LDD1537 | [2] |
| LDCM0302 | AC40 | HEK-293T | C296(1.24) | LDD1541 | [2] |
| LDCM0307 | AC45 | HEK-293T | C296(1.15) | LDD1546 | [2] |
| LDCM0310 | AC48 | HEK-293T | C296(1.36) | LDD1549 | [2] |
| LDCM0312 | AC5 | HEK-293T | C296(1.04) | LDD1551 | [2] |
| LDCM0316 | AC53 | HEK-293T | C296(0.96) | LDD1555 | [2] |
| LDCM0319 | AC56 | HEK-293T | C296(1.21) | LDD1558 | [2] |
| LDCM0325 | AC61 | HEK-293T | C296(0.90) | LDD1564 | [2] |
| LDCM0328 | AC64 | HEK-293T | C296(1.13) | LDD1567 | [2] |
| LDCM0345 | AC8 | HEK-293T | C296(1.57) | LDD1569 | [2] |
| LDCM0248 | AKOS034007472 | HEK-293T | C296(0.92) | LDD1511 | [2] |
| LDCM0275 | AKOS034007705 | HEK-293T | C296(0.98) | LDD1514 | [2] |
| LDCM0367 | CL1 | HEK-293T | C296(1.25) | LDD1571 | [2] |
| LDCM0370 | CL101 | HEK-293T | C296(1.20) | LDD1574 | [2] |
| LDCM0371 | CL102 | HEK-293T | C296(1.02) | LDD1575 | [2] |
| LDCM0372 | CL103 | HEK-293T | C296(0.97) | LDD1576 | [2] |
| LDCM0374 | CL105 | HEK-293T | C296(0.98) | LDD1578 | [2] |
| LDCM0375 | CL106 | HEK-293T | C296(1.01) | LDD1579 | [2] |
| LDCM0376 | CL107 | HEK-293T | C296(0.97) | LDD1580 | [2] |
| LDCM0378 | CL109 | HEK-293T | C296(0.98) | LDD1582 | [2] |
| LDCM0380 | CL110 | HEK-293T | C296(1.20) | LDD1584 | [2] |
| LDCM0381 | CL111 | HEK-293T | C296(0.94) | LDD1585 | [2] |
| LDCM0383 | CL113 | HEK-293T | C296(1.39) | LDD1587 | [2] |
| LDCM0384 | CL114 | HEK-293T | C296(1.03) | LDD1588 | [2] |
| LDCM0385 | CL115 | HEK-293T | C296(0.94) | LDD1589 | [2] |
| LDCM0387 | CL117 | HEK-293T | C296(0.91) | LDD1591 | [2] |
| LDCM0388 | CL118 | HEK-293T | C296(0.95) | LDD1592 | [2] |
| LDCM0389 | CL119 | HEK-293T | C296(0.88) | LDD1593 | [2] |
| LDCM0390 | CL12 | HEK-293T | C296(1.49) | LDD1594 | [2] |
| LDCM0392 | CL121 | HEK-293T | C296(1.01) | LDD1596 | [2] |
| LDCM0393 | CL122 | HEK-293T | C296(1.18) | LDD1597 | [2] |
| LDCM0394 | CL123 | HEK-293T | C296(1.04) | LDD1598 | [2] |
| LDCM0396 | CL125 | HEK-293T | C296(1.24) | LDD1600 | [2] |
| LDCM0397 | CL126 | HEK-293T | C296(1.12) | LDD1601 | [2] |
| LDCM0398 | CL127 | HEK-293T | C296(1.15) | LDD1602 | [2] |
| LDCM0400 | CL13 | HEK-293T | C296(1.17) | LDD1604 | [2] |
| LDCM0401 | CL14 | HEK-293T | C296(1.05) | LDD1605 | [2] |
| LDCM0402 | CL15 | HEK-293T | C296(1.13) | LDD1606 | [2] |
| LDCM0407 | CL2 | HEK-293T | C296(1.08) | LDD1611 | [2] |
| LDCM0409 | CL21 | HEK-293T | C296(1.39) | LDD1613 | [2] |
| LDCM0412 | CL24 | HEK-293T | C296(1.25) | LDD1616 | [2] |
| LDCM0413 | CL25 | HEK-293T | C296(1.16) | LDD1617 | [2] |
| LDCM0414 | CL26 | HEK-293T | C296(1.24) | LDD1618 | [2] |
| LDCM0415 | CL27 | HEK-293T | C296(0.95) | LDD1619 | [2] |
| LDCM0418 | CL3 | HEK-293T | C296(1.21) | LDD1622 | [2] |
| LDCM0422 | CL33 | HEK-293T | C296(1.36) | LDD1626 | [2] |
| LDCM0425 | CL36 | HEK-293T | C296(1.08) | LDD1629 | [2] |
| LDCM0426 | CL37 | HEK-293T | C296(1.32) | LDD1630 | [2] |
| LDCM0428 | CL39 | HEK-293T | C296(1.04) | LDD1632 | [2] |
| LDCM0435 | CL45 | HEK-293T | C296(0.92) | LDD1639 | [2] |
| LDCM0438 | CL48 | HEK-293T | C296(1.51) | LDD1642 | [2] |
| LDCM0439 | CL49 | HEK-293T | C296(1.47) | LDD1643 | [2] |
| LDCM0441 | CL50 | HEK-293T | C296(0.93) | LDD1645 | [2] |
| LDCM0448 | CL57 | HEK-293T | C296(1.05) | LDD1651 | [2] |
| LDCM0452 | CL60 | HEK-293T | C296(1.54) | LDD1655 | [2] |
| LDCM0453 | CL61 | HEK-293T | C296(1.01) | LDD1656 | [2] |
| LDCM0454 | CL62 | HEK-293T | C296(1.01) | LDD1657 | [2] |
| LDCM0455 | CL63 | HEK-293T | C296(0.72) | LDD1658 | [2] |
| LDCM0461 | CL69 | HEK-293T | C296(1.39) | LDD1664 | [2] |
| LDCM0465 | CL72 | HEK-293T | C296(1.35) | LDD1668 | [2] |
| LDCM0466 | CL73 | HEK-293T | C296(1.58) | LDD1669 | [2] |
| LDCM0467 | CL74 | HEK-293T | C296(1.02) | LDD1670 | [2] |
| LDCM0475 | CL81 | HEK-293T | C296(1.03) | LDD1678 | [2] |
| LDCM0478 | CL84 | HEK-293T | C296(1.06) | LDD1681 | [2] |
| LDCM0479 | CL85 | HEK-293T | C296(0.94) | LDD1682 | [2] |
| LDCM0480 | CL86 | HEK-293T | C296(1.02) | LDD1683 | [2] |
| LDCM0481 | CL87 | HEK-293T | C296(1.22) | LDD1684 | [2] |
| LDCM0484 | CL9 | HEK-293T | C296(0.94) | LDD1687 | [2] |
| LDCM0488 | CL93 | HEK-293T | C296(1.37) | LDD1691 | [2] |
| LDCM0491 | CL96 | HEK-293T | C296(1.69) | LDD1694 | [2] |
| LDCM0492 | CL97 | HEK-293T | C296(1.10) | LDD1695 | [2] |
| LDCM0493 | CL98 | HEK-293T | C296(1.04) | LDD1696 | [2] |
| LDCM0494 | CL99 | HEK-293T | C296(0.98) | LDD1697 | [2] |
| LDCM0495 | E2913 | HEK-293T | C296(0.99) | LDD1698 | [2] |
| LDCM0625 | F8 | Ramos | C346(1.86) | LDD2187 | [1] |
| LDCM0572 | Fragment10 | Ramos | C346(1.46) | LDD2189 | [1] |
| LDCM0573 | Fragment11 | Ramos | C346(13.88) | LDD2190 | [1] |
| LDCM0575 | Fragment13 | Ramos | C346(1.32) | LDD2192 | [1] |
| LDCM0580 | Fragment21 | Ramos | C346(1.31) | LDD2195 | [1] |
| LDCM0582 | Fragment23 | Ramos | C346(0.62) | LDD2196 | [1] |
| LDCM0578 | Fragment27 | Ramos | C346(0.77) | LDD2197 | [1] |
| LDCM0586 | Fragment28 | Ramos | C346(1.31) | LDD2198 | [1] |
| LDCM0588 | Fragment30 | Ramos | C346(1.99) | LDD2199 | [1] |
| LDCM0589 | Fragment31 | Ramos | C346(1.13) | LDD2200 | [1] |
| LDCM0590 | Fragment32 | Ramos | C346(1.82) | LDD2201 | [1] |
| LDCM0468 | Fragment33 | HEK-293T | C296(1.04) | LDD1671 | [2] |
| LDCM0596 | Fragment38 | Ramos | C346(2.60) | LDD2203 | [1] |
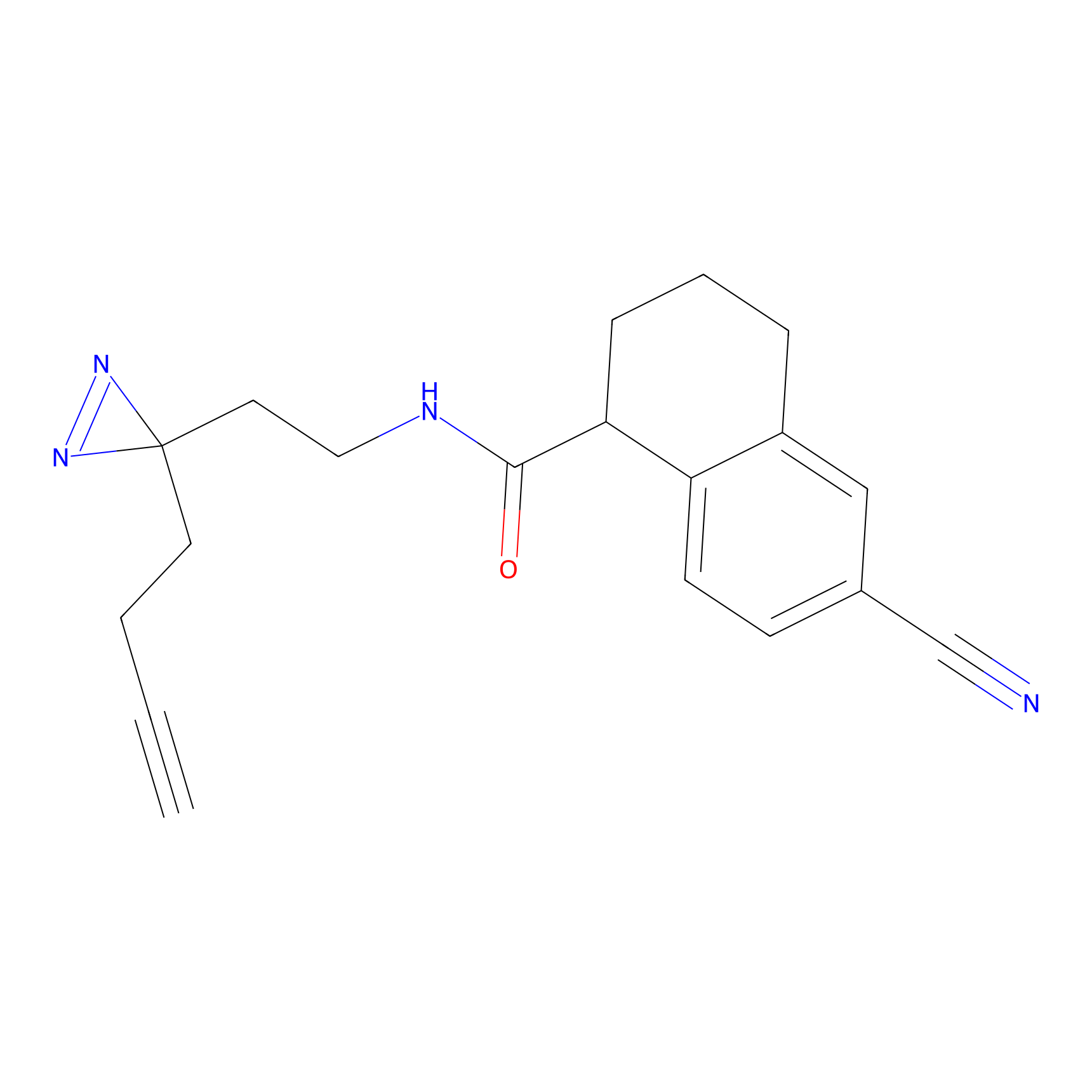
| LDCM0566 | Fragment4 | Ramos | C346(5.16) | LDD2184 | [1] |
| LDCM0427 | Fragment51 | HEK-293T | C296(1.07) | LDD1631 | [2] |
| LDCM0610 | Fragment52 | Ramos | C346(1.45) | LDD2204 | [1] |
| LDCM0614 | Fragment56 | Ramos | C346(1.04) | LDD2205 | [1] |
The Interaction Atlas With This Target
The Protein(s) Related To This Target
Enzyme
| Protein name | Family | Uniprot ID | |||
|---|---|---|---|---|---|
| Ubiquitin-conjugating enzyme E2 J1 (UBE2J1) | Ubiquitin-conjugating enzyme family | Q9Y385 | |||
Transporter and channel
Other
| Protein name | Family | Uniprot ID | |||
|---|---|---|---|---|---|
| Keratin-associated protein 10-6 (KRTAP10-6) | KRTAP type 10 family | P60371 | |||
References