Details of the Target
General Information of Target
| Target ID | LDTP13192 | |||||
|---|---|---|---|---|---|---|
| Target Name | Tight junction protein ZO-2 (TJP2) | |||||
| Gene Name | TJP2 | |||||
| Gene ID | 9414 | |||||
| Synonyms |
X104; ZO2; Tight junction protein ZO-2; Tight junction protein 2; Zona occludens protein 2; Zonula occludens protein 2 |
|||||
| 3D Structure | ||||||
| Sequence |
MSSRVGDLSPQQQEALARFRENLQDLLPILPNADDYFLLRWLRARNFDLQKSEDMLRRHM
EFRKQQDLDNIVTWQPPEVIQLYDSGGLCGYDYEGCPVYFNIIGSLDPKGLLLSASKQDM IRKRIKVCELLLHECELQTQKLGRKIEMALMVFDMEGLSLKHLWKPAVEVYQQFFSILEA NYPETLKNLIVIRAPKLFPVAFNLVKSFMSEETRRKIVILGDNWKQELTKFISPDQLPVE FGGTMTDPDGNPKCLTKINYGGEVPKSYYLCEQVRLQYEHTRSVGRGSSLQVENEILFPG CVLRWQFASDGGDIGFGVFLKTKMGEQQSAREMTEVLPSQRYNAHMVPEDGSLTCLQAGV YVLRFDNTYSRMHAKKLSYTVEVLLPDKASEETLQSLKAMRPSPTQ |
|||||
| Target Bioclass |
Other
|
|||||
| Family |
MAGUK family
|
|||||
| Subcellular location |
Cell junction, adherens junction
|
|||||
| Function | Plays a role in tight junctions and adherens junctions. Acts as a positive regulator of RANKL-induced osteoclast differentiation, potentially via mediating downstream transcriptional activity. | |||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Target Site Mutations in Different Cell Lines
| Cell line | Mutation details | Probe for labeling this protein in this cell | |||
|---|---|---|---|---|---|
| G415 | SNV: p.E262K | . | |||
| HCT116 | Deletion: p.T849RfsTer12 | . | |||
| HCT15 | SNV: p.A906T | . | |||
| HEC1 | SNV: p.H181R; p.Y261C | DBIA Probe Info | |||
| HEC1B | SNV: p.H181R | . | |||
| HT115 | SNV: p.E403D | . | |||
| HT3 | SNV: p.P1146S | DBIA Probe Info | |||
| HUPT3 | SNV: p.A647S | DBIA Probe Info | |||
| IGROV1 | SNV: p.R183W | . | |||
| JURKAT | SNV: p.A683V | . | |||
| KNS42 | SNV: p.A1040V | . | |||
| KYSE150 | SNV: p.D915N | DBIA Probe Info | |||
| KYSE30 | SNV: p.P967S | . | |||
| LNCaP clone FGC | Deletion: p.R167AfsTer144 SNV: p.S713I |
. | |||
| LS180 | Deletion: p.T849RfsTer12 | DBIA Probe Info | |||
| MFE319 | SNV: p.A740V | DBIA Probe Info | |||
| NALM6 | SNV: p.E960Ter | . | |||
| REH | SNV: p.R187Q | . | |||
| RL | SNV: p.Q675L | . | |||
| SKMEL3 | Insertion: p.D1008_Y1013dup | . | |||
| SKNSH | SNV: p.R193L | . | |||
| SKOV3 | SNV: p.D258G | . | |||
| SW480 | SNV: p.N396I | . | |||
| WM2664 | Insertion: p.E968RfsTer11 | . | |||
Probe(s) Labeling This Target
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
|
m-APA Probe Info |
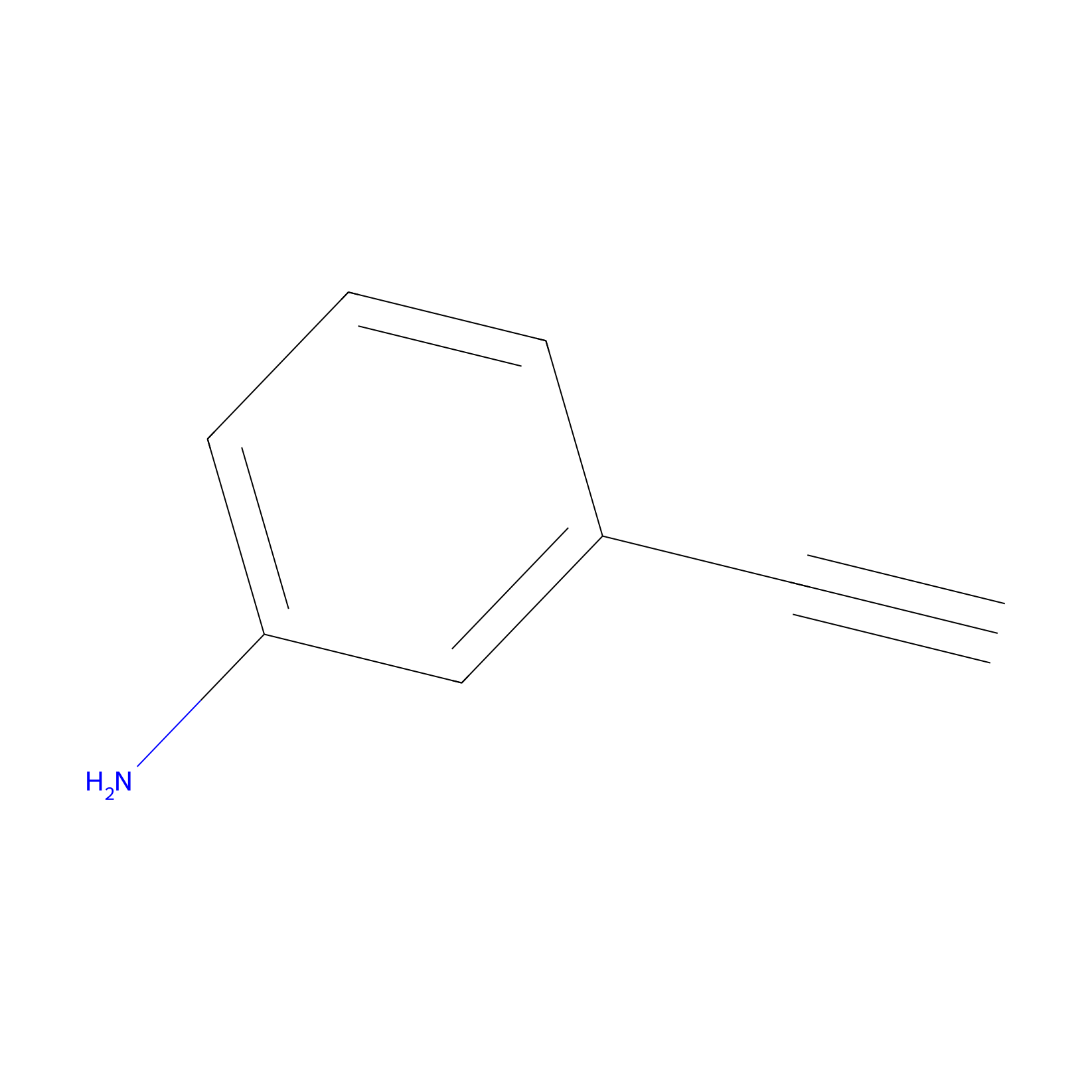 |
15.00 | LDD0402 | [1] | |
|
CY-1 Probe Info |
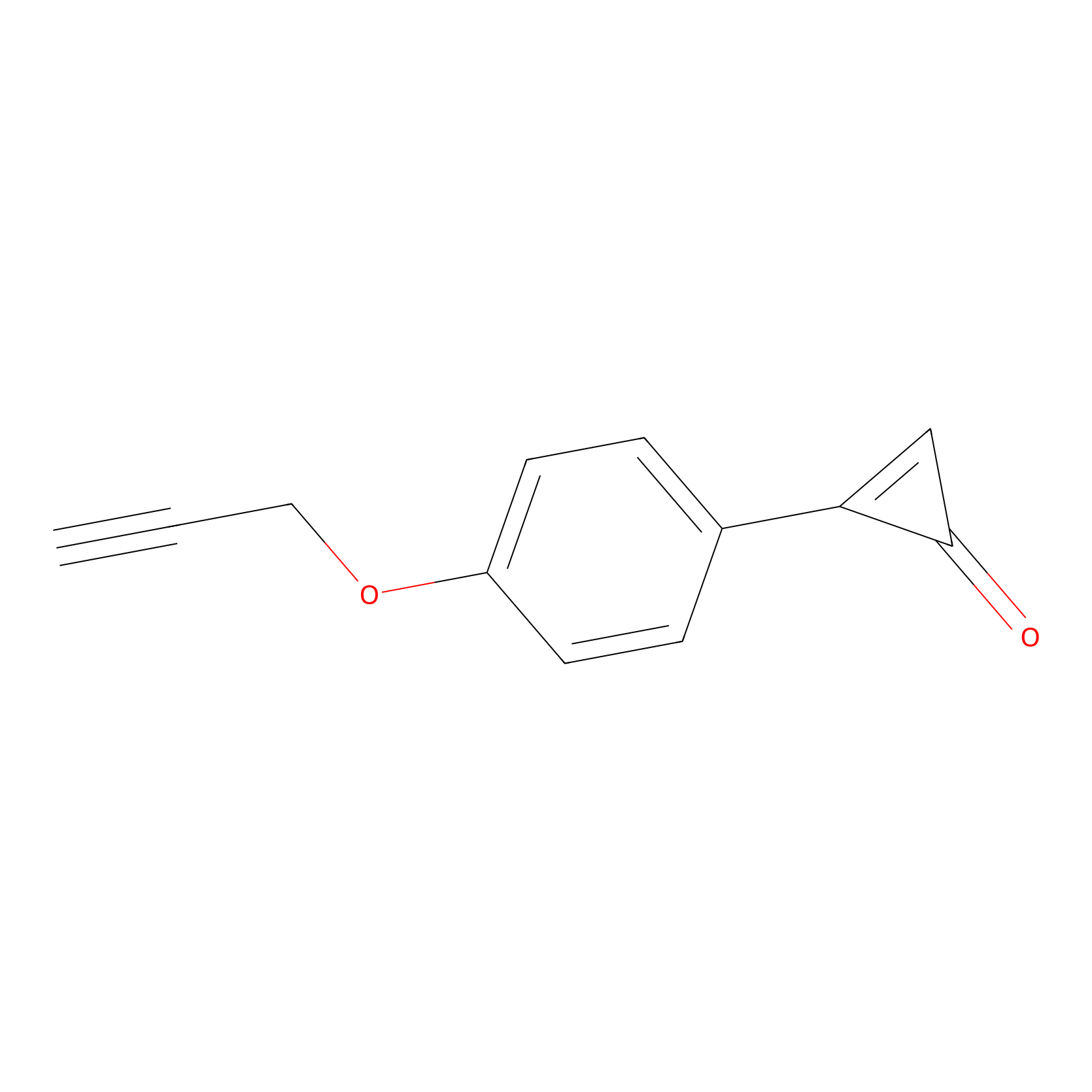 |
100.00 | LDD0243 | [2] | |
|
CY4 Probe Info |
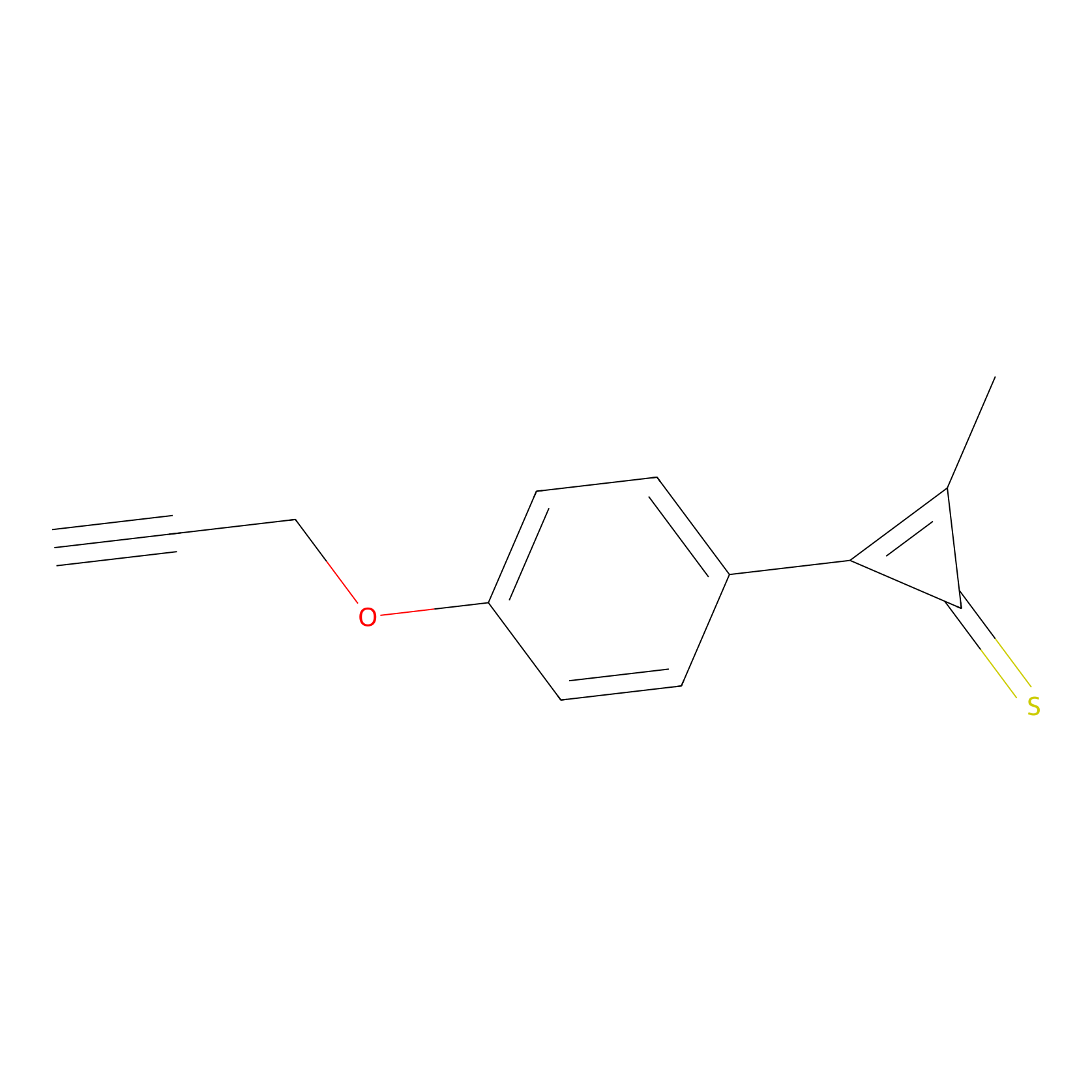 |
100.00 | LDD0244 | [2] | |
|
W1 Probe Info |
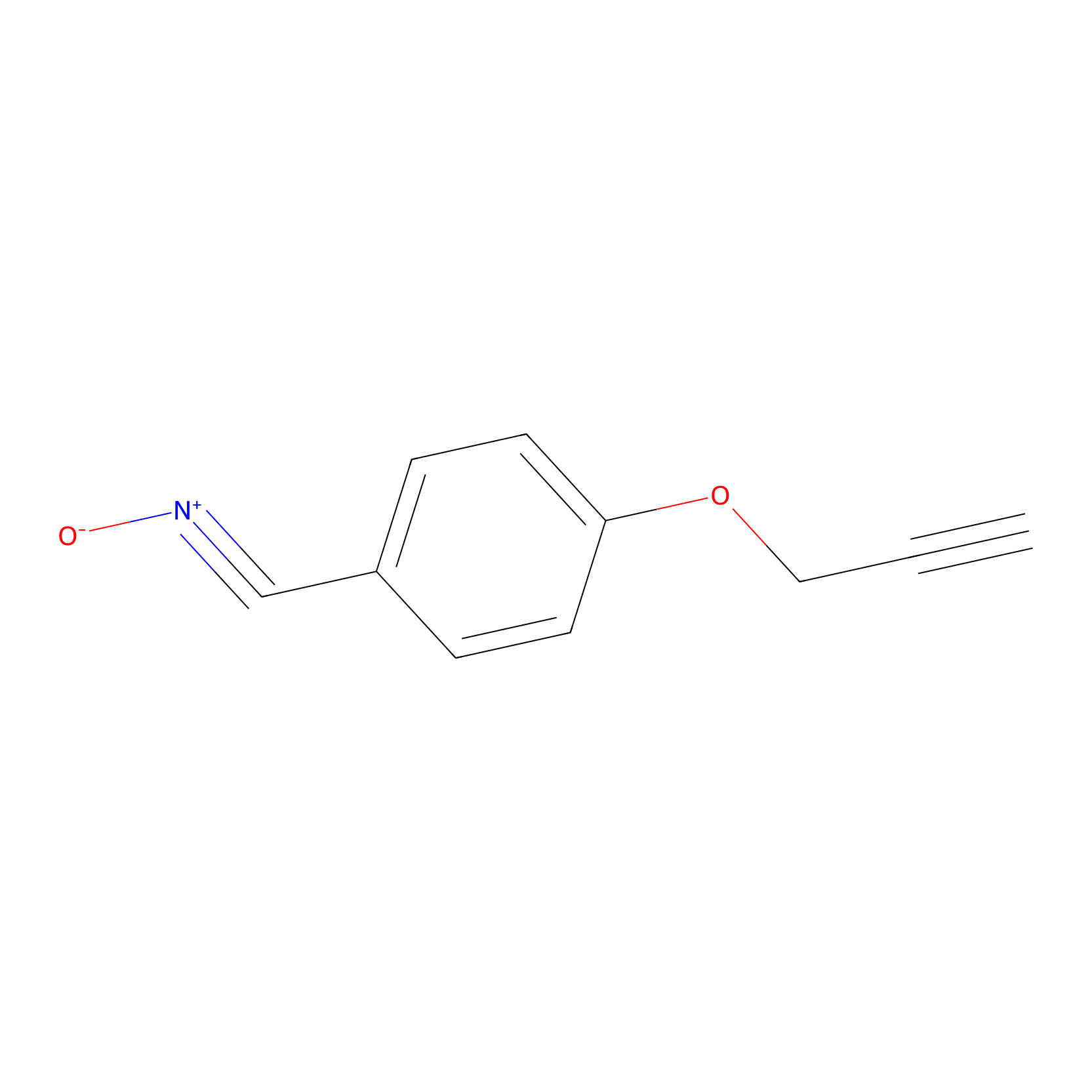 |
10.19 | LDD0235 | [3] | |
|
STPyne Probe Info |
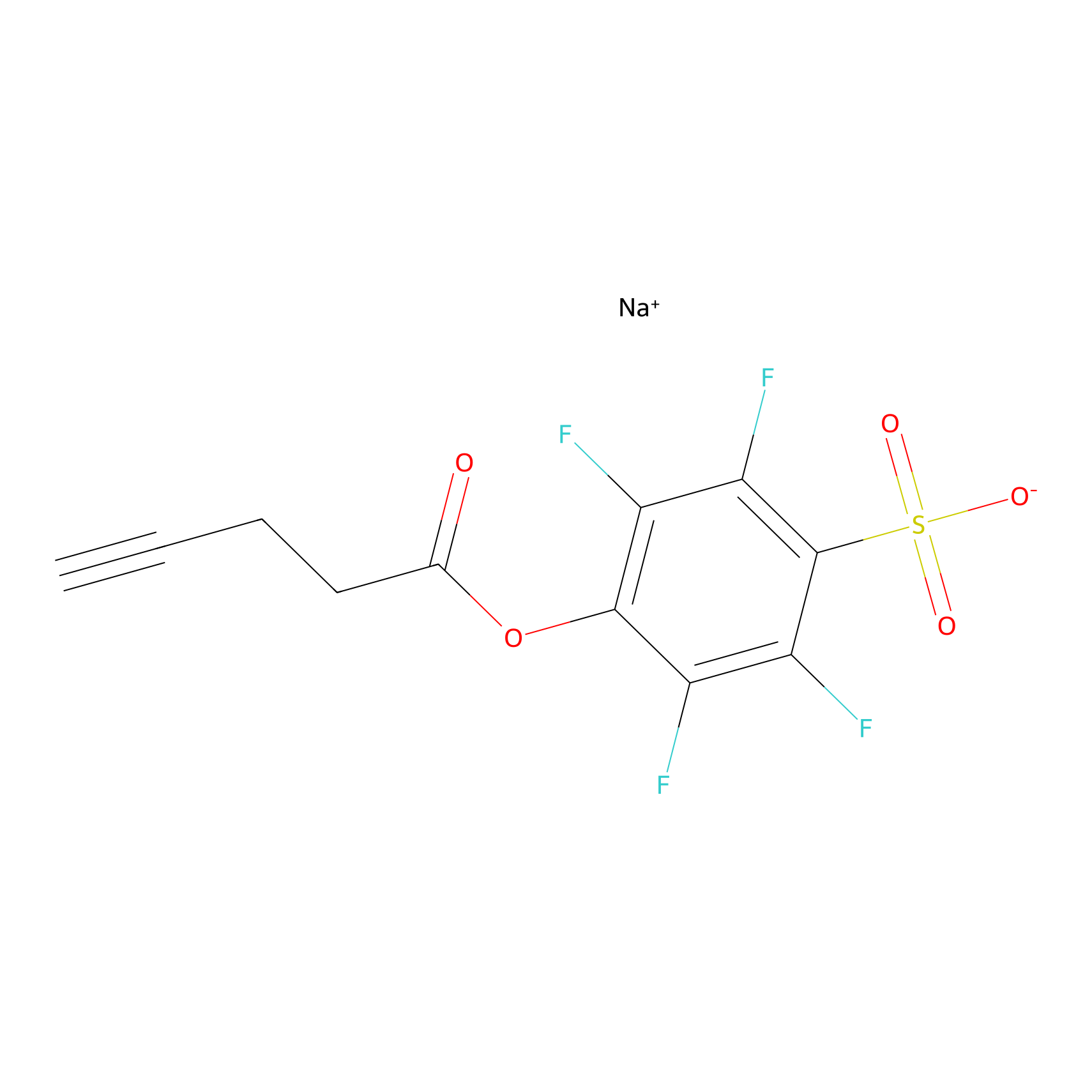 |
K1042(10.00); K1087(4.33); K1091(2.58); K1113(8.59) | LDD0277 | [4] | |
|
ONAyne Probe Info |
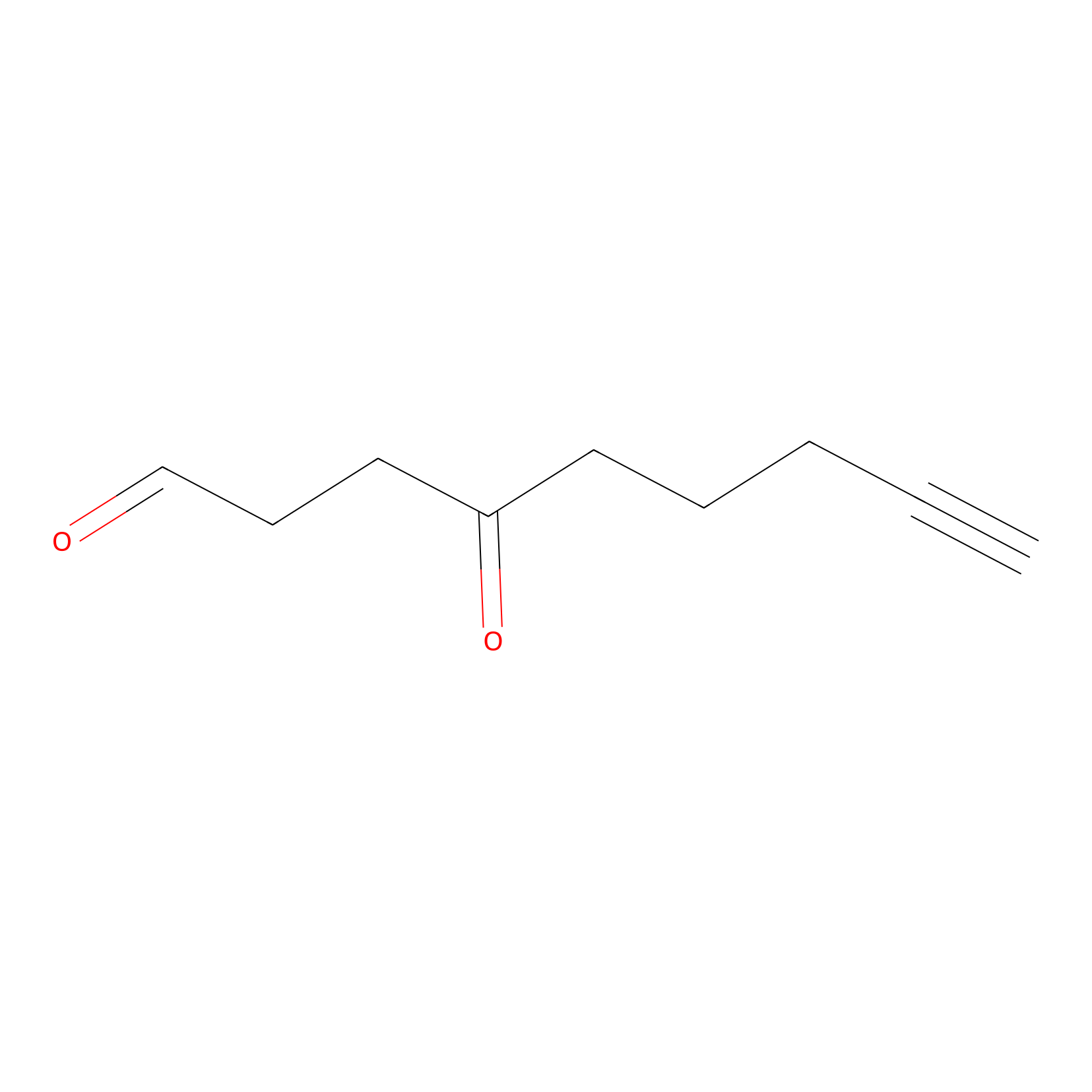 |
K845(10.00) | LDD0275 | [4] | |
|
Probe 1 Probe Info |
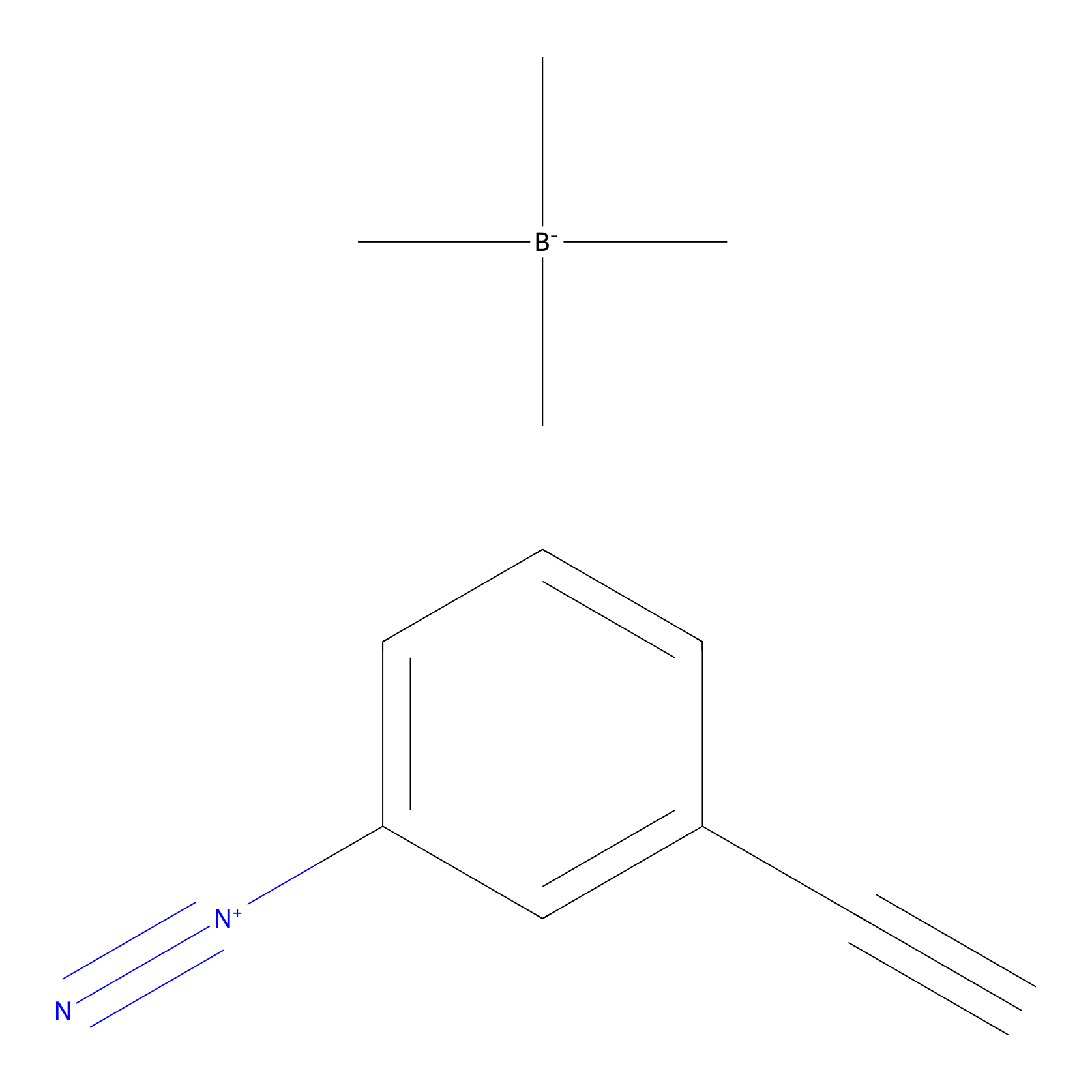 |
Y249(27.58); Y257(10.41); Y261(19.30); Y265(26.35) | LDD3495 | [5] | |
|
DBIA Probe Info |
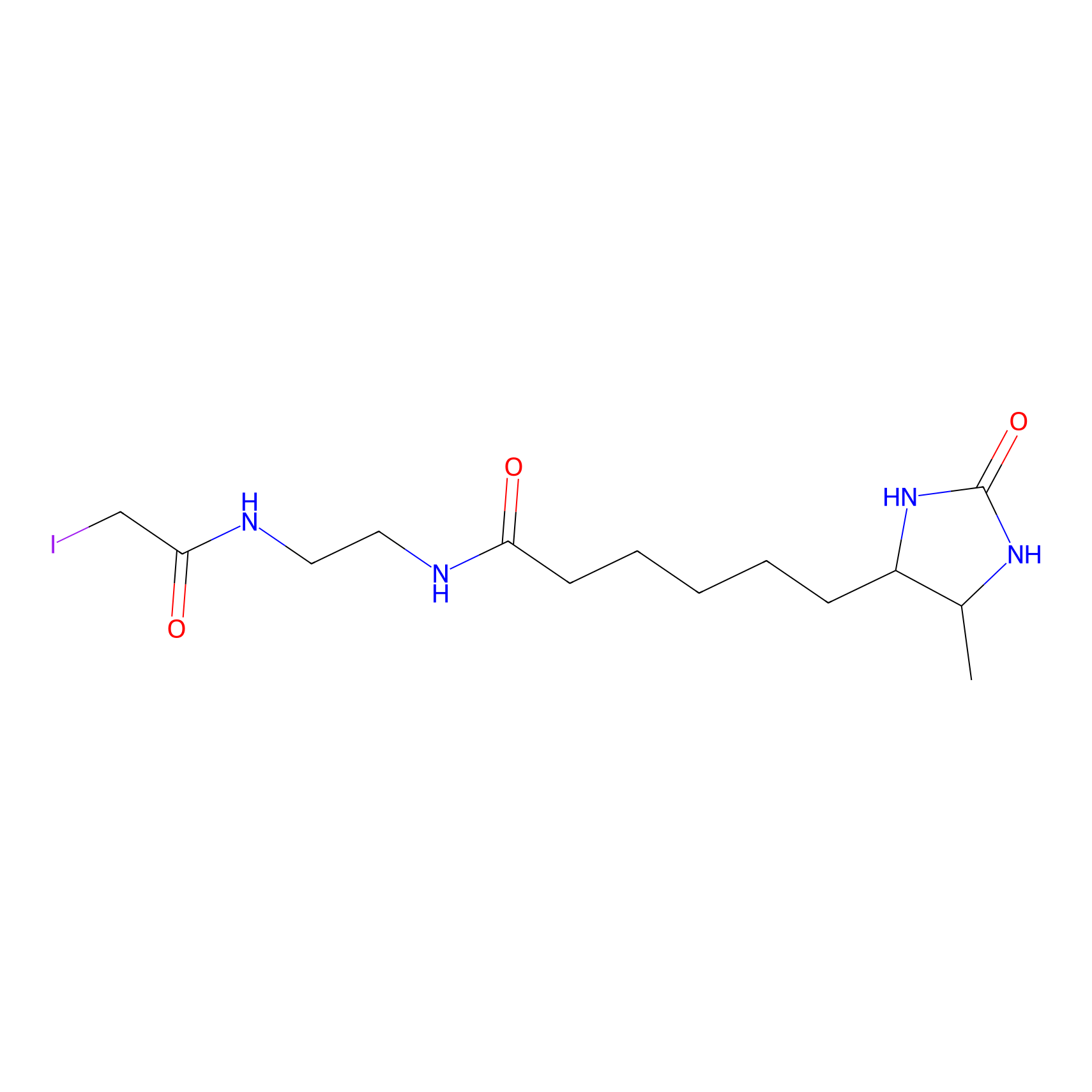 |
C945(1.66) | LDD3312 | [6] | |
|
BTD Probe Info |
 |
C615(2.19) | LDD1700 | [7] | |
|
AHL-Pu-1 Probe Info |
 |
C914(2.37) | LDD0171 | [8] | |
|
HHS-475 Probe Info |
 |
Y423(0.74) | LDD0264 | [9] | |
|
5E-2FA Probe Info |
 |
H877(0.00); H1134(0.00) | LDD2235 | [10] | |
|
N1 Probe Info |
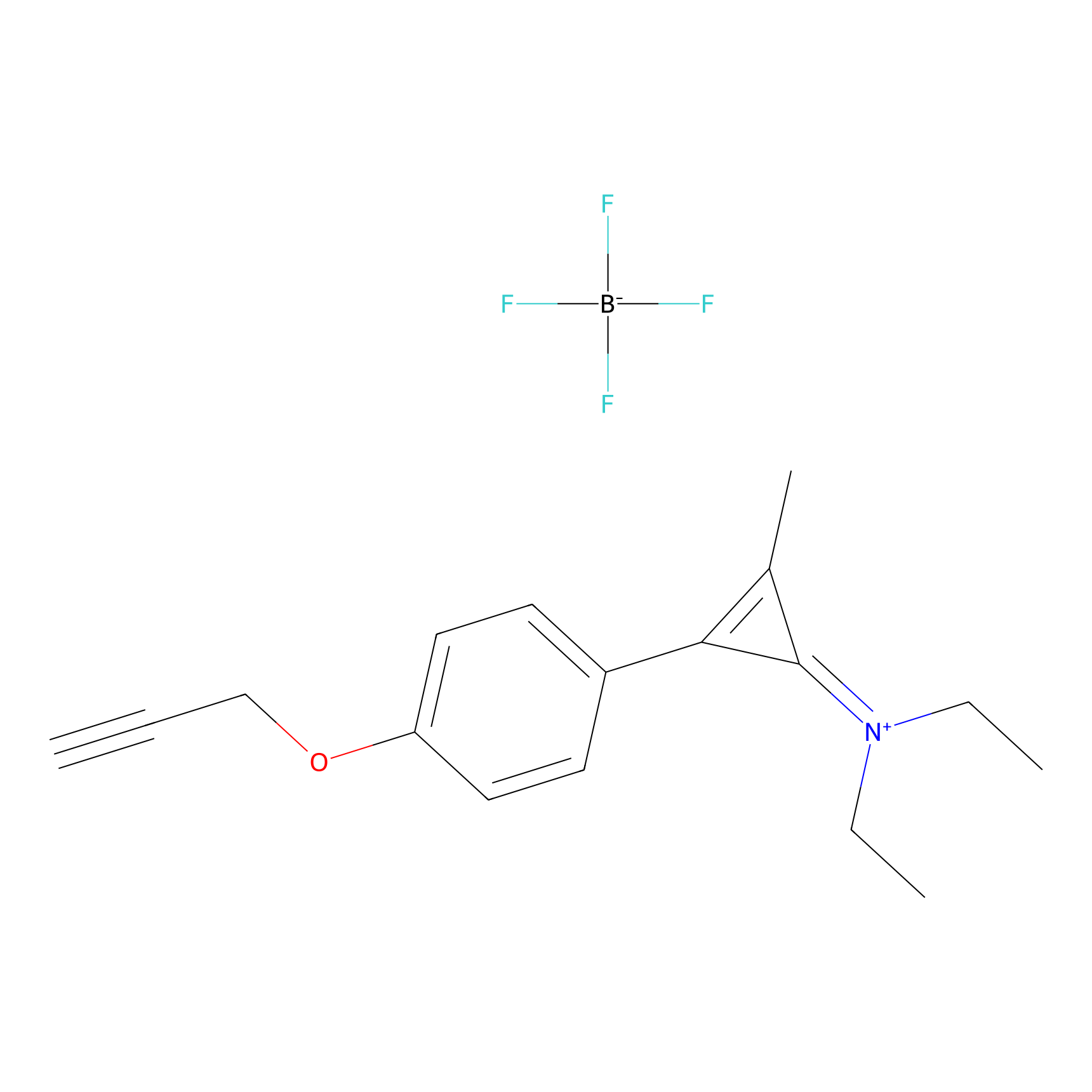 |
N.A. | LDD0245 | [2] | |
|
IA-alkyne Probe Info |
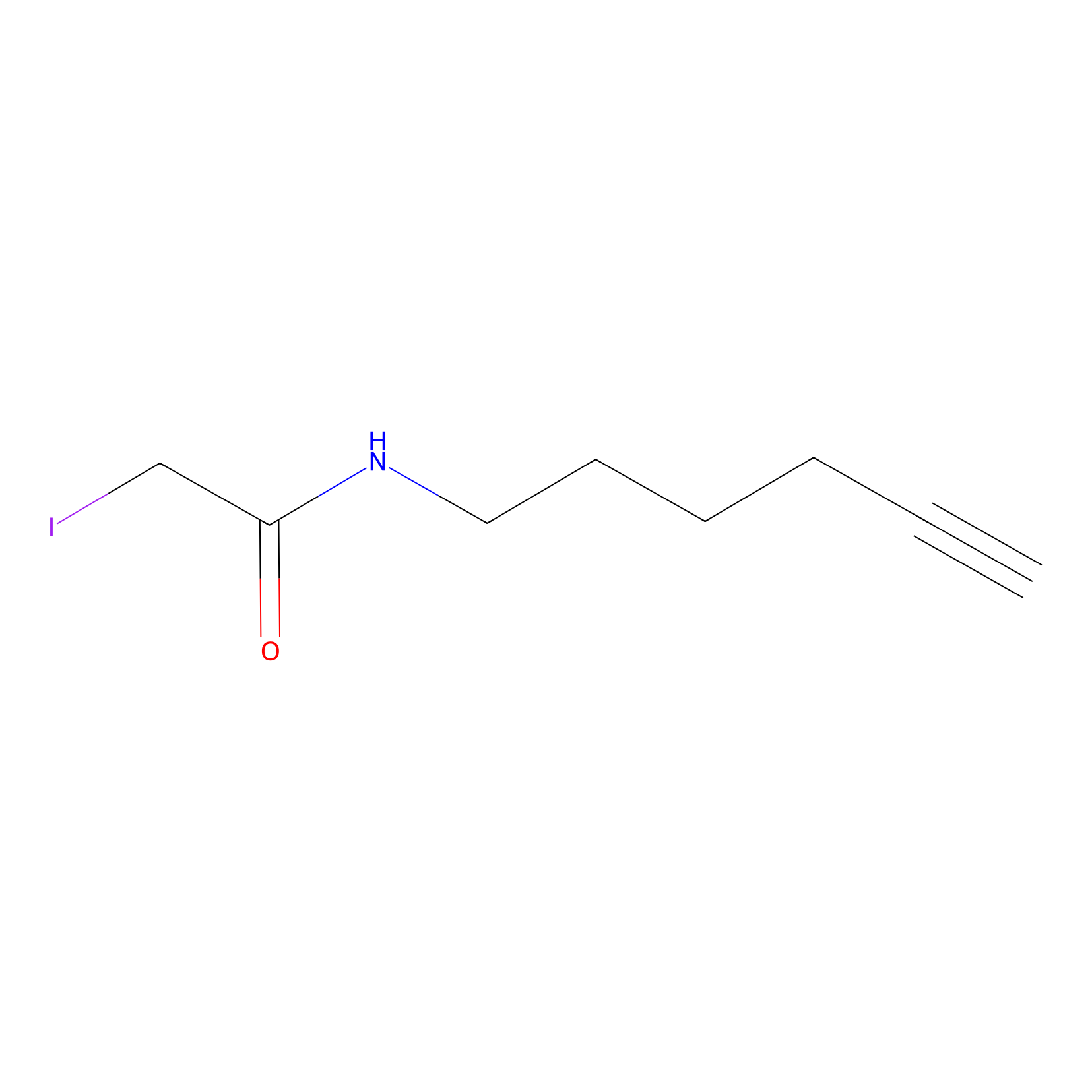 |
C601(0.00); C615(0.00) | LDD0162 | [11] | |
|
ATP probe Probe Info |
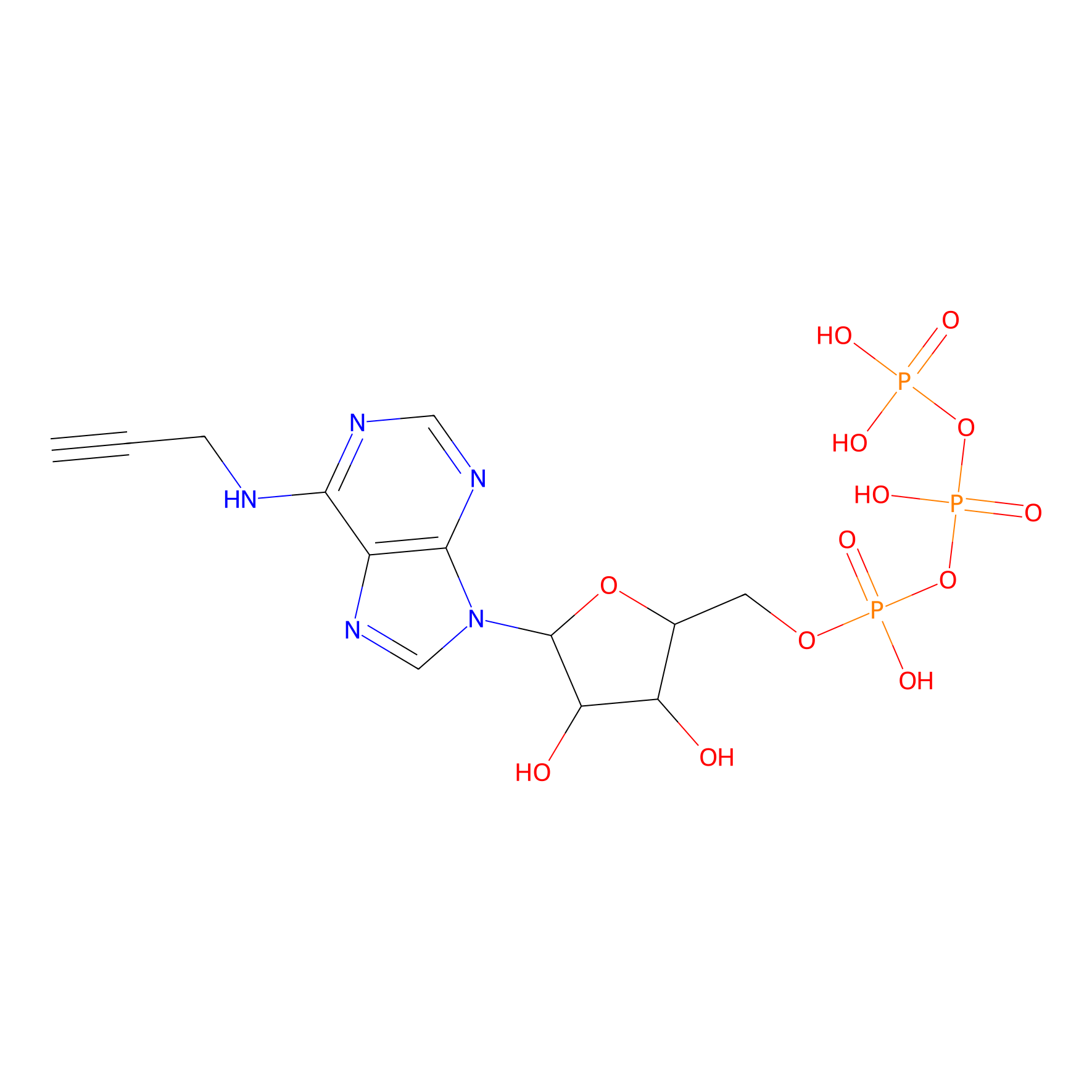 |
N.A. | LDD0035 | [12] | |
|
IPM Probe Info |
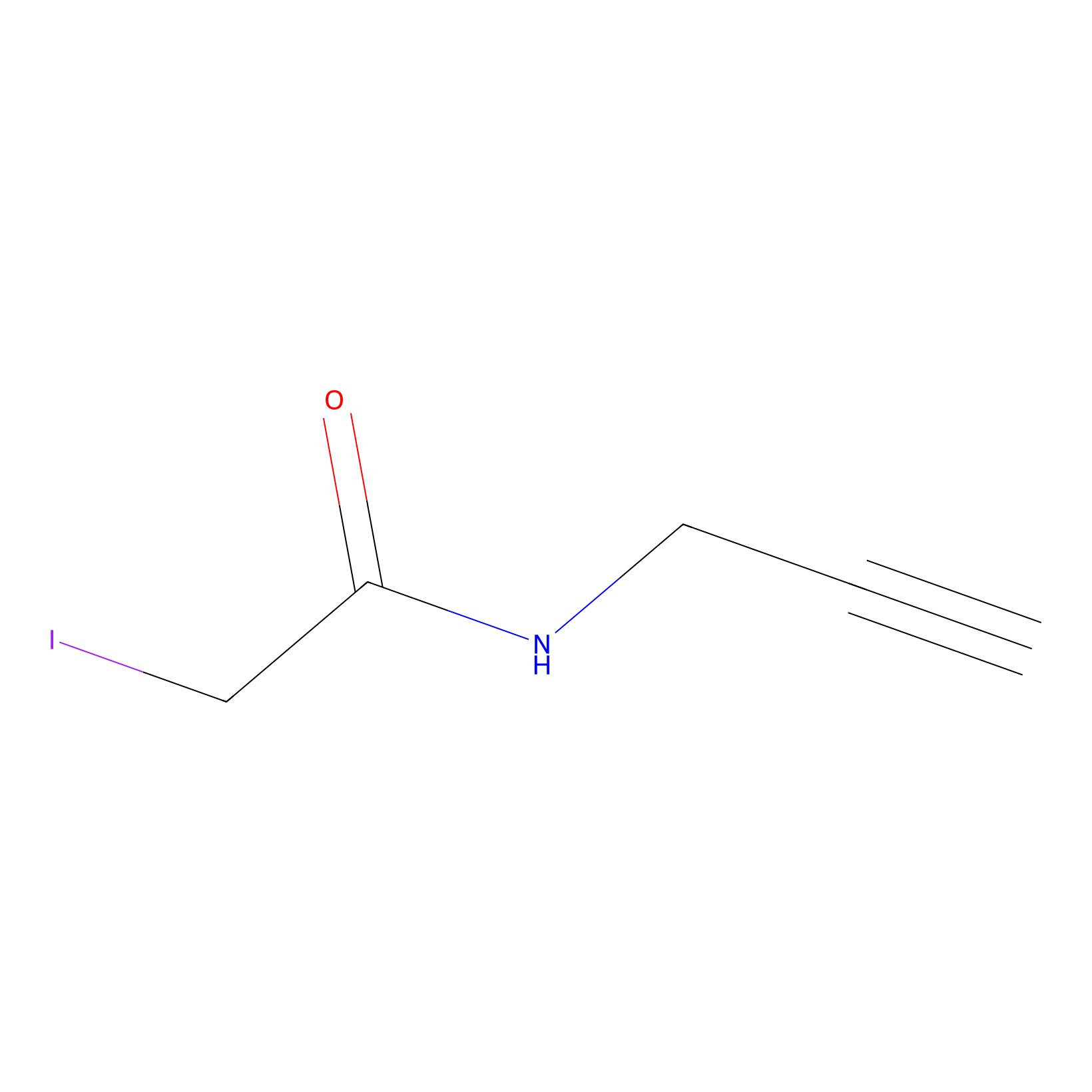 |
C601(0.00); C615(0.00) | LDD0147 | [13] | |
|
OSF Probe Info |
 |
N.A. | LDD0029 | [14] | |
|
SF Probe Info |
 |
Y261(0.00); Y1035(0.00) | LDD0028 | [14] | |
|
TFBX Probe Info |
 |
C615(0.00); C601(0.00) | LDD0148 | [13] | |
|
Phosphinate-6 Probe Info |
 |
C615(0.00); C601(0.00) | LDD0018 | [15] | |
|
1d-yne Probe Info |
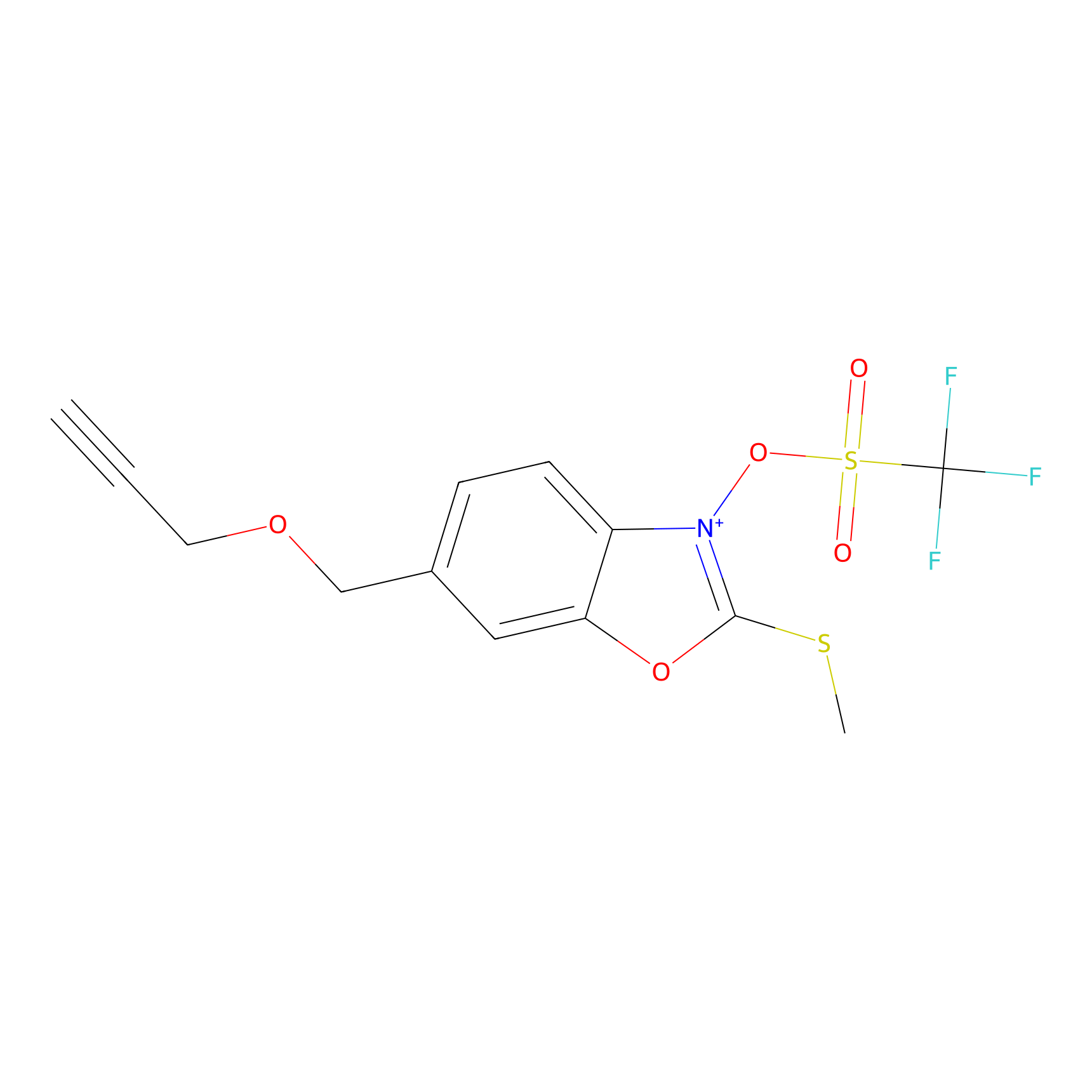 |
N.A. | LDD0357 | [16] | |
|
NAIA_5 Probe Info |
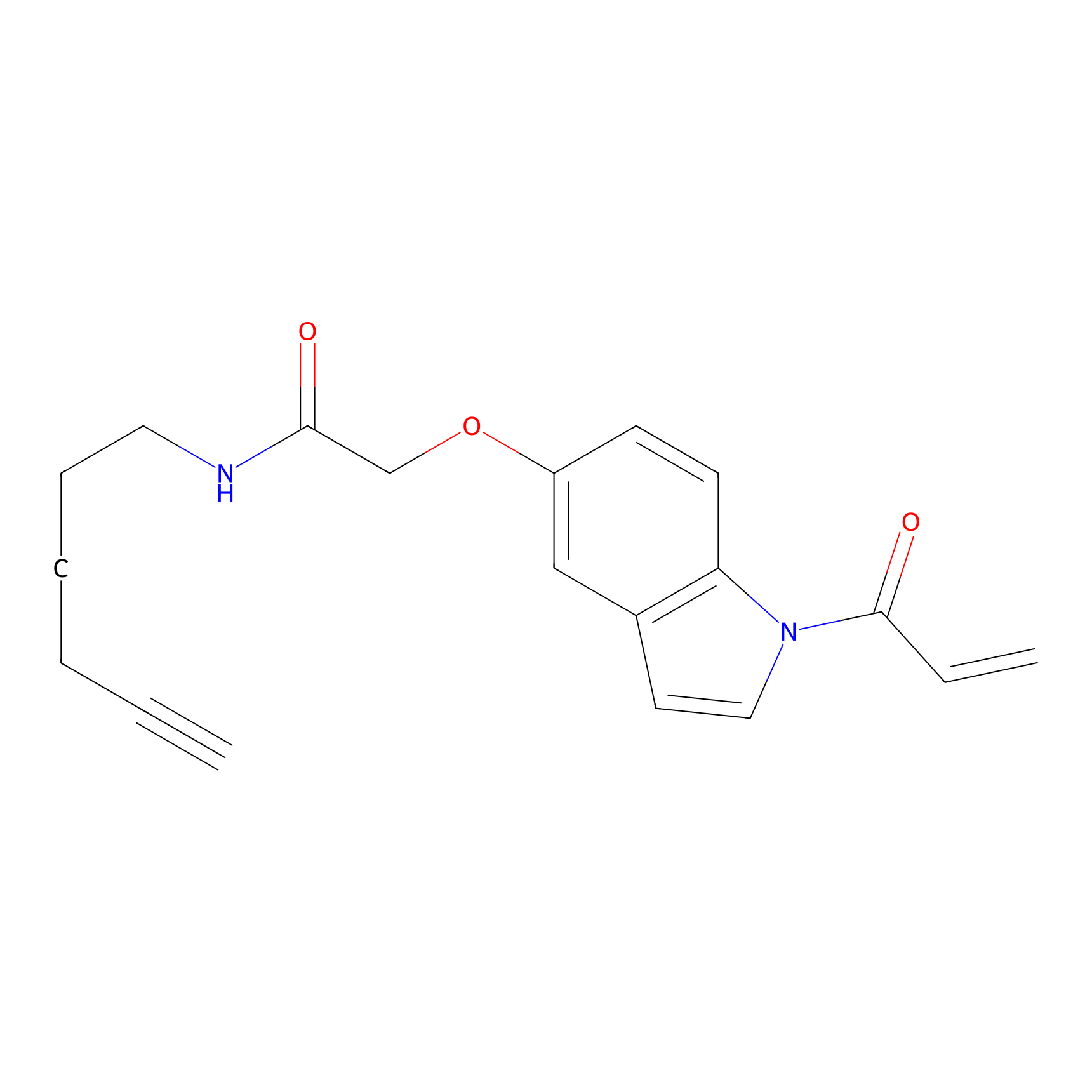 |
C601(0.00); C914(0.00); C615(0.00) | LDD2223 | [17] | |
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0524 | 2-Cyano-N-(2-morpholin-4-yl-ethyl)-acetamide | MDA-MB-231 | C601(0.95) | LDD2117 | [7] |
| LDCM0558 | 2-Cyano-N-phenylacetamide | MDA-MB-231 | C615(1.84); C601(1.28) | LDD2152 | [7] |
| LDCM0510 | 3-(4-(Hydroxydiphenylmethyl)piperidin-1-yl)-3-oxopropanenitrile | MDA-MB-231 | C601(1.03) | LDD2103 | [7] |
| LDCM0538 | 4-(Cyanoacetyl)morpholine | MDA-MB-231 | C615(0.91) | LDD2131 | [7] |
| LDCM0025 | 4SU-RNA | HEK-293T | C914(2.41) | LDD0172 | [8] |
| LDCM0026 | 4SU-RNA+native RNA | DM93 | C914(2.37) | LDD0171 | [8] |
| LDCM0214 | AC1 | HEK-293T | C601(0.97); C914(1.05); C850(0.99) | LDD1507 | [18] |
| LDCM0215 | AC10 | HEK-293T | C601(0.82); C914(0.99); C850(0.90) | LDD1508 | [18] |
| LDCM0226 | AC11 | HEK-293T | C615(0.98); C601(0.94); C914(0.98); C850(0.89) | LDD1509 | [18] |
| LDCM0237 | AC12 | HEK-293T | C615(1.00); C601(0.90); C914(0.93); C850(0.98) | LDD1510 | [18] |
| LDCM0259 | AC14 | HEK-293T | C615(1.04); C601(0.94); C914(1.02); C850(0.95) | LDD1512 | [18] |
| LDCM0270 | AC15 | HEK-293T | C615(1.08); C601(0.88); C914(0.89); C850(1.01) | LDD1513 | [18] |
| LDCM0276 | AC17 | HEK-293T | C601(0.91); C914(0.97); C850(0.94) | LDD1515 | [18] |
| LDCM0277 | AC18 | HEK-293T | C601(0.85); C914(0.92); C850(0.95) | LDD1516 | [18] |
| LDCM0278 | AC19 | HEK-293T | C615(0.93); C601(0.94); C914(0.90); C850(0.87) | LDD1517 | [18] |
| LDCM0279 | AC2 | HEK-293T | C601(0.78); C914(0.85); C850(1.00) | LDD1518 | [18] |
| LDCM0280 | AC20 | HEK-293T | C615(1.03); C601(0.91); C914(0.97); C850(1.06) | LDD1519 | [18] |
| LDCM0281 | AC21 | HEK-293T | C615(0.83); C601(0.96); C914(1.06); C850(0.97) | LDD1520 | [18] |
| LDCM0282 | AC22 | HEK-293T | C615(0.99); C601(0.96); C914(0.94); C850(1.04) | LDD1521 | [18] |
| LDCM0283 | AC23 | HEK-293T | C615(0.97); C601(0.84); C914(0.91); C850(0.93) | LDD1522 | [18] |
| LDCM0284 | AC24 | HEK-293T | C615(0.95); C601(0.94); C914(1.16); C850(0.82) | LDD1523 | [18] |
| LDCM0285 | AC25 | HEK-293T | C601(1.03); C914(0.96); C850(0.87) | LDD1524 | [18] |
| LDCM0286 | AC26 | HEK-293T | C601(0.90); C914(0.88); C850(1.09) | LDD1525 | [18] |
| LDCM0287 | AC27 | HEK-293T | C615(0.94); C601(0.98); C914(1.01); C850(1.05) | LDD1526 | [18] |
| LDCM0288 | AC28 | HEK-293T | C615(1.02); C601(0.97); C914(1.02); C850(1.03) | LDD1527 | [18] |
| LDCM0289 | AC29 | HEK-293T | C615(1.01); C601(0.98); C914(0.90); C850(1.10) | LDD1528 | [18] |
| LDCM0290 | AC3 | HEK-293T | C615(1.00); C601(0.93); C914(0.93); C850(1.11) | LDD1529 | [18] |
| LDCM0291 | AC30 | HEK-293T | C615(1.03); C601(0.96); C914(0.77); C850(1.00) | LDD1530 | [18] |
| LDCM0292 | AC31 | HEK-293T | C615(0.98); C601(0.91); C914(1.00); C850(1.08) | LDD1531 | [18] |
| LDCM0293 | AC32 | HEK-293T | C615(0.95); C601(0.98); C914(1.02); C850(1.03) | LDD1532 | [18] |
| LDCM0294 | AC33 | HEK-293T | C601(0.89); C914(1.07); C850(0.91) | LDD1533 | [18] |
| LDCM0295 | AC34 | HEK-293T | C601(0.80); C914(1.01); C850(0.98) | LDD1534 | [18] |
| LDCM0296 | AC35 | HEK-293T | C615(0.90); C601(0.89); C914(1.09); C850(1.00) | LDD1535 | [18] |
| LDCM0297 | AC36 | HEK-293T | C615(1.07); C601(0.85); C914(0.98); C850(0.92) | LDD1536 | [18] |
| LDCM0298 | AC37 | HEK-293T | C615(0.92); C601(0.91); C914(0.95); C850(1.02) | LDD1537 | [18] |
| LDCM0299 | AC38 | HEK-293T | C615(1.05); C601(0.92); C914(1.34); C850(0.98) | LDD1538 | [18] |
| LDCM0300 | AC39 | HEK-293T | C615(1.12); C601(0.83); C914(1.02); C850(1.01) | LDD1539 | [18] |
| LDCM0301 | AC4 | HEK-293T | C615(1.06); C601(0.91); C914(0.97); C850(1.06) | LDD1540 | [18] |
| LDCM0302 | AC40 | HEK-293T | C615(1.07); C601(0.95); C914(1.06); C850(0.96) | LDD1541 | [18] |
| LDCM0303 | AC41 | HEK-293T | C601(0.81); C914(0.91); C850(1.03) | LDD1542 | [18] |
| LDCM0304 | AC42 | HEK-293T | C601(0.79); C914(1.21); C850(0.89) | LDD1543 | [18] |
| LDCM0305 | AC43 | HEK-293T | C615(0.92); C601(0.88); C914(0.95); C850(0.93) | LDD1544 | [18] |
| LDCM0306 | AC44 | HEK-293T | C615(1.03); C601(0.86); C914(0.98); C850(1.03) | LDD1545 | [18] |
| LDCM0307 | AC45 | HEK-293T | C615(1.03); C601(0.91); C914(0.91); C850(1.06) | LDD1546 | [18] |
| LDCM0308 | AC46 | HEK-293T | C615(1.06); C601(0.94); C914(1.12); C850(1.01) | LDD1547 | [18] |
| LDCM0309 | AC47 | HEK-293T | C615(1.10); C601(0.91); C914(1.02); C850(0.91) | LDD1548 | [18] |
| LDCM0310 | AC48 | HEK-293T | C615(0.91); C601(0.91); C914(1.02); C850(0.90) | LDD1549 | [18] |
| LDCM0311 | AC49 | HEK-293T | C601(0.96); C914(1.01); C850(0.90) | LDD1550 | [18] |
| LDCM0312 | AC5 | HEK-293T | C615(0.95); C601(0.89); C914(1.11); C850(0.97) | LDD1551 | [18] |
| LDCM0313 | AC50 | HEK-293T | C601(0.81); C914(0.99); C850(0.99) | LDD1552 | [18] |
| LDCM0314 | AC51 | HEK-293T | C615(0.99); C601(0.96); C914(1.00); C850(0.96) | LDD1553 | [18] |
| LDCM0315 | AC52 | HEK-293T | C615(1.02); C601(0.90); C914(1.00); C850(0.96) | LDD1554 | [18] |
| LDCM0316 | AC53 | HEK-293T | C615(1.03); C601(0.94); C914(1.02); C850(1.07) | LDD1555 | [18] |
| LDCM0317 | AC54 | HEK-293T | C615(1.06); C601(0.93); C914(0.95); C850(1.06) | LDD1556 | [18] |
| LDCM0318 | AC55 | HEK-293T | C615(1.09); C601(0.91); C914(0.94); C850(1.21) | LDD1557 | [18] |
| LDCM0319 | AC56 | HEK-293T | C615(0.99); C601(0.92); C914(1.12); C850(0.95) | LDD1558 | [18] |
| LDCM0320 | AC57 | HEK-293T | C601(0.94); C914(0.97); C850(0.88) | LDD1559 | [18] |
| LDCM0321 | AC58 | HEK-293T | C601(0.81); C914(1.13); C850(0.97) | LDD1560 | [18] |
| LDCM0322 | AC59 | HEK-293T | C615(1.07); C601(0.92); C914(0.98); C850(1.03) | LDD1561 | [18] |
| LDCM0323 | AC6 | HEK-293T | C615(1.06); C601(0.96); C914(0.80); C850(1.05) | LDD1562 | [18] |
| LDCM0324 | AC60 | HEK-293T | C615(0.95); C601(0.91); C914(0.97); C850(1.04) | LDD1563 | [18] |
| LDCM0325 | AC61 | HEK-293T | C615(0.84); C601(0.88); C914(0.95); C850(1.11) | LDD1564 | [18] |
| LDCM0326 | AC62 | HEK-293T | C615(1.04); C601(0.98); C914(0.90); C850(1.06) | LDD1565 | [18] |
| LDCM0327 | AC63 | HEK-293T | C615(1.01); C601(0.87); C914(0.85); C850(1.05) | LDD1566 | [18] |
| LDCM0328 | AC64 | HEK-293T | C615(0.98); C601(0.95); C914(0.84); C850(0.95) | LDD1567 | [18] |
| LDCM0334 | AC7 | HEK-293T | C615(1.03); C601(0.86); C914(0.93); C850(1.05) | LDD1568 | [18] |
| LDCM0345 | AC8 | HEK-293T | C615(1.02); C601(0.92); C914(0.91); C850(0.92) | LDD1569 | [18] |
| LDCM0545 | Acetamide | MDA-MB-231 | C615(0.37) | LDD2138 | [7] |
| LDCM0248 | AKOS034007472 | HEK-293T | C615(0.83); C601(0.91); C914(0.86); C850(0.94) | LDD1511 | [18] |
| LDCM0356 | AKOS034007680 | HEK-293T | C601(0.89); C914(0.98); C850(0.91) | LDD1570 | [18] |
| LDCM0275 | AKOS034007705 | HEK-293T | C615(1.01); C601(0.94); C914(0.96); C850(0.94) | LDD1514 | [18] |
| LDCM0498 | BS-3668 | MDA-MB-231 | C615(0.79) | LDD2091 | [7] |
| LDCM0632 | CL-Sc | Hep-G2 | C601(3.06) | LDD2227 | [17] |
| LDCM0367 | CL1 | HEK-293T | C615(0.96); C601(0.89); C914(0.83); C850(0.92) | LDD1571 | [18] |
| LDCM0368 | CL10 | HEK-293T | C615(1.29); C601(0.82); C914(0.77); C850(0.84) | LDD1572 | [18] |
| LDCM0369 | CL100 | HEK-293T | C615(1.04); C601(0.85); C914(0.99); C850(0.89) | LDD1573 | [18] |
| LDCM0370 | CL101 | HEK-293T | C615(0.88); C601(1.01); C914(1.03); C850(0.98) | LDD1574 | [18] |
| LDCM0371 | CL102 | HEK-293T | C615(1.06); C601(0.83); C914(0.94); C850(1.04) | LDD1575 | [18] |
| LDCM0372 | CL103 | HEK-293T | C601(0.86); C914(0.87); C850(1.08) | LDD1576 | [18] |
| LDCM0373 | CL104 | HEK-293T | C615(1.02); C601(0.89); C914(0.91); C850(1.12) | LDD1577 | [18] |
| LDCM0374 | CL105 | HEK-293T | C615(0.94); C601(0.96); C914(0.95); C850(1.04) | LDD1578 | [18] |
| LDCM0375 | CL106 | HEK-293T | C615(0.87); C601(0.92); C914(0.94); C850(1.01) | LDD1579 | [18] |
| LDCM0376 | CL107 | HEK-293T | C601(0.86); C914(0.81); C850(1.23) | LDD1580 | [18] |
| LDCM0377 | CL108 | HEK-293T | C615(0.93); C601(0.90); C914(1.08); C850(1.21) | LDD1581 | [18] |
| LDCM0378 | CL109 | HEK-293T | C615(0.87); C601(1.02); C914(0.83); C850(0.98) | LDD1582 | [18] |
| LDCM0379 | CL11 | HEK-293T | C615(1.32); C601(0.86); C914(0.89); C850(0.88) | LDD1583 | [18] |
| LDCM0380 | CL110 | HEK-293T | C615(1.06); C601(0.83); C914(1.04); C850(0.79) | LDD1584 | [18] |
| LDCM0381 | CL111 | HEK-293T | C601(0.89); C914(0.84); C850(1.04) | LDD1585 | [18] |
| LDCM0382 | CL112 | HEK-293T | C615(0.91); C601(0.95); C914(1.00); C850(1.11) | LDD1586 | [18] |
| LDCM0383 | CL113 | HEK-293T | C615(0.97); C601(0.95); C914(1.28); C850(0.97) | LDD1587 | [18] |
| LDCM0384 | CL114 | HEK-293T | C615(0.93); C601(0.82); C914(0.96); C850(0.93) | LDD1588 | [18] |
| LDCM0385 | CL115 | HEK-293T | C601(0.94); C914(0.99); C850(0.96) | LDD1589 | [18] |
| LDCM0386 | CL116 | HEK-293T | C615(0.90); C601(0.92); C914(1.06); C850(0.98) | LDD1590 | [18] |
| LDCM0387 | CL117 | HEK-293T | C615(1.01); C601(0.92); C914(0.93); C850(1.03) | LDD1591 | [18] |
| LDCM0388 | CL118 | HEK-293T | C615(1.05); C601(0.88); C914(1.04); C850(1.09) | LDD1592 | [18] |
| LDCM0389 | CL119 | HEK-293T | C601(0.91); C914(0.81); C850(1.12) | LDD1593 | [18] |
| LDCM0390 | CL12 | HEK-293T | C615(1.15); C601(0.99); C914(1.03); C850(0.96) | LDD1594 | [18] |
| LDCM0391 | CL120 | HEK-293T | C615(0.94); C601(0.95); C914(1.08); C850(1.01) | LDD1595 | [18] |
| LDCM0392 | CL121 | HEK-293T | C615(1.08); C601(0.89); C914(0.80); C850(1.01) | LDD1596 | [18] |
| LDCM0393 | CL122 | HEK-293T | C615(0.88); C601(0.88); C914(0.81); C850(1.07) | LDD1597 | [18] |
| LDCM0394 | CL123 | HEK-293T | C601(0.83); C914(0.91); C850(0.98) | LDD1598 | [18] |
| LDCM0395 | CL124 | HEK-293T | C615(0.97); C601(0.92); C914(0.93); C850(1.20) | LDD1599 | [18] |
| LDCM0396 | CL125 | HEK-293T | C615(0.95); C601(0.95); C914(0.89); C850(0.98) | LDD1600 | [18] |
| LDCM0397 | CL126 | HEK-293T | C615(0.95); C601(0.93); C914(0.97); C850(0.98) | LDD1601 | [18] |
| LDCM0398 | CL127 | HEK-293T | C601(0.85); C914(0.99); C850(0.85) | LDD1602 | [18] |
| LDCM0399 | CL128 | HEK-293T | C615(0.94); C601(0.93); C914(0.97); C850(1.03) | LDD1603 | [18] |
| LDCM0400 | CL13 | HEK-293T | C615(1.21); C601(0.90); C914(1.01); C850(0.96) | LDD1604 | [18] |
| LDCM0401 | CL14 | HEK-293T | C615(0.94); C601(0.79); C914(1.22); C850(1.00) | LDD1605 | [18] |
| LDCM0402 | CL15 | HEK-293T | C601(0.74); C914(1.09); C850(1.05) | LDD1606 | [18] |
| LDCM0403 | CL16 | HEK-293T | C615(0.90); C601(0.88); C914(1.04); C850(1.12) | LDD1607 | [18] |
| LDCM0404 | CL17 | HEK-293T | C601(0.81); C914(1.00); C850(0.84) | LDD1608 | [18] |
| LDCM0405 | CL18 | HEK-293T | C601(0.77); C914(1.01); C850(0.97) | LDD1609 | [18] |
| LDCM0406 | CL19 | HEK-293T | C615(1.17); C601(0.88); C914(1.01); C850(0.97) | LDD1610 | [18] |
| LDCM0407 | CL2 | HEK-293T | C615(1.02); C601(0.83); C914(0.98); C850(1.13) | LDD1611 | [18] |
| LDCM0408 | CL20 | HEK-293T | C615(1.12); C601(0.89); C914(1.05); C850(0.91) | LDD1612 | [18] |
| LDCM0409 | CL21 | HEK-293T | C615(0.97); C601(0.86); C914(0.95); C850(0.94) | LDD1613 | [18] |
| LDCM0410 | CL22 | HEK-293T | C615(1.13); C601(0.97); C914(0.93); C850(1.03) | LDD1614 | [18] |
| LDCM0411 | CL23 | HEK-293T | C615(1.18); C601(0.87); C914(0.84); C850(0.98) | LDD1615 | [18] |
| LDCM0412 | CL24 | HEK-293T | C615(1.13); C601(1.03); C914(1.05); C850(0.93) | LDD1616 | [18] |
| LDCM0413 | CL25 | HEK-293T | C615(1.37); C601(0.88); C914(0.84); C850(0.96) | LDD1617 | [18] |
| LDCM0414 | CL26 | HEK-293T | C615(0.95); C601(0.89); C914(0.98); C850(1.02) | LDD1618 | [18] |
| LDCM0415 | CL27 | HEK-293T | C601(0.90); C914(0.92); C850(1.03) | LDD1619 | [18] |
| LDCM0416 | CL28 | HEK-293T | C615(0.97); C601(0.87); C914(1.02); C850(1.09) | LDD1620 | [18] |
| LDCM0417 | CL29 | HEK-293T | C601(0.89); C914(0.84); C850(0.85) | LDD1621 | [18] |
| LDCM0418 | CL3 | HEK-293T | C601(0.84); C914(1.11); C850(1.10) | LDD1622 | [18] |
| LDCM0419 | CL30 | HEK-293T | C601(0.81); C914(0.85); C850(0.91) | LDD1623 | [18] |
| LDCM0420 | CL31 | HEK-293T | C615(1.02); C601(0.94); C914(0.92); C850(0.92) | LDD1624 | [18] |
| LDCM0421 | CL32 | HEK-293T | C615(1.07); C601(0.93); C914(0.89); C850(0.99) | LDD1625 | [18] |
| LDCM0422 | CL33 | HEK-293T | C615(1.12); C601(0.85); C914(0.87); C850(0.87) | LDD1626 | [18] |
| LDCM0423 | CL34 | HEK-293T | C615(1.06); C601(0.97); C914(0.95); C850(1.01) | LDD1627 | [18] |
| LDCM0424 | CL35 | HEK-293T | C615(1.26); C601(0.92); C914(0.78); C850(0.99) | LDD1628 | [18] |
| LDCM0425 | CL36 | HEK-293T | C615(1.04); C601(1.06); C914(1.01); C850(0.87) | LDD1629 | [18] |
| LDCM0426 | CL37 | HEK-293T | C615(0.80); C601(0.93); C914(0.83); C850(0.98) | LDD1630 | [18] |
| LDCM0428 | CL39 | HEK-293T | C601(0.84); C914(1.06); C850(1.06) | LDD1632 | [18] |
| LDCM0429 | CL4 | HEK-293T | C615(0.99); C601(0.77); C914(1.05); C850(0.90) | LDD1633 | [18] |
| LDCM0430 | CL40 | HEK-293T | C615(0.94); C601(0.92); C914(1.05); C850(1.03) | LDD1634 | [18] |
| LDCM0431 | CL41 | HEK-293T | C601(0.92); C914(0.89); C850(0.94) | LDD1635 | [18] |
| LDCM0432 | CL42 | HEK-293T | C601(0.85); C914(0.87); C850(0.95) | LDD1636 | [18] |
| LDCM0433 | CL43 | HEK-293T | C615(1.05); C601(0.94); C914(0.91); C850(0.99) | LDD1637 | [18] |
| LDCM0434 | CL44 | HEK-293T | C615(1.05); C601(0.94); C914(0.91); C850(0.97) | LDD1638 | [18] |
| LDCM0435 | CL45 | HEK-293T | C615(1.09); C601(0.99); C914(1.10); C850(0.65) | LDD1639 | [18] |
| LDCM0436 | CL46 | HEK-293T | C615(1.07); C601(1.00); C914(0.77); C850(0.98) | LDD1640 | [18] |
| LDCM0437 | CL47 | HEK-293T | C615(1.12); C601(0.97); C914(0.85); C850(0.93) | LDD1641 | [18] |
| LDCM0438 | CL48 | HEK-293T | C615(1.10); C601(0.98); C914(1.16); C850(0.98) | LDD1642 | [18] |
| LDCM0439 | CL49 | HEK-293T | C615(0.87); C601(0.90); C914(0.66); C850(1.07) | LDD1643 | [18] |
| LDCM0440 | CL5 | HEK-293T | C601(0.83); C914(0.98); C850(0.93) | LDD1644 | [18] |
| LDCM0441 | CL50 | HEK-293T | C615(0.96); C601(0.85); C914(1.15); C850(1.09) | LDD1645 | [18] |
| LDCM0443 | CL52 | HEK-293T | C615(1.03); C601(0.87); C914(1.08); C850(1.07) | LDD1646 | [18] |
| LDCM0444 | CL53 | HEK-293T | C601(0.83); C914(0.98); C850(0.95) | LDD1647 | [18] |
| LDCM0445 | CL54 | HEK-293T | C601(0.70); C914(0.86); C850(0.90) | LDD1648 | [18] |
| LDCM0446 | CL55 | HEK-293T | C615(1.17); C601(0.91); C914(1.00); C850(1.03) | LDD1649 | [18] |
| LDCM0447 | CL56 | HEK-293T | C615(1.08); C601(0.94); C914(1.06); C850(1.04) | LDD1650 | [18] |
| LDCM0448 | CL57 | HEK-293T | C615(0.98); C601(0.89); C914(1.06); C850(0.88) | LDD1651 | [18] |
| LDCM0449 | CL58 | HEK-293T | C615(1.10); C601(0.92); C914(0.84); C850(1.07) | LDD1652 | [18] |
| LDCM0450 | CL59 | HEK-293T | C615(1.22); C601(0.85); C914(1.13); C850(0.98) | LDD1653 | [18] |
| LDCM0451 | CL6 | HEK-293T | C601(0.75); C914(0.90); C850(0.92) | LDD1654 | [18] |
| LDCM0452 | CL60 | HEK-293T | C615(1.13); C601(0.96); C914(1.16); C850(0.93) | LDD1655 | [18] |
| LDCM0453 | CL61 | HEK-293T | C615(0.84); C601(0.94); C914(0.80); C850(1.04) | LDD1656 | [18] |
| LDCM0454 | CL62 | HEK-293T | C615(1.11); C601(0.93); C914(1.18); C850(1.10) | LDD1657 | [18] |
| LDCM0455 | CL63 | HEK-293T | C601(0.89); C914(0.91); C850(1.13) | LDD1658 | [18] |
| LDCM0456 | CL64 | HEK-293T | C615(1.00); C601(0.85); C914(0.98); C850(0.85) | LDD1659 | [18] |
| LDCM0457 | CL65 | HEK-293T | C601(0.82); C914(0.97); C850(0.97) | LDD1660 | [18] |
| LDCM0458 | CL66 | HEK-293T | C601(0.81); C914(0.87); C850(0.97) | LDD1661 | [18] |
| LDCM0459 | CL67 | HEK-293T | C615(1.05); C601(0.93); C914(0.95); C850(0.91) | LDD1662 | [18] |
| LDCM0460 | CL68 | HEK-293T | C615(1.06); C601(0.98); C914(0.97); C850(0.89) | LDD1663 | [18] |
| LDCM0461 | CL69 | HEK-293T | C615(1.11); C601(0.91); C914(0.87); C850(0.89) | LDD1664 | [18] |
| LDCM0462 | CL7 | HEK-293T | C615(1.14); C601(0.87); C914(0.96); C850(1.03) | LDD1665 | [18] |
| LDCM0463 | CL70 | HEK-293T | C615(1.09); C601(1.03); C914(0.93); C850(0.94) | LDD1666 | [18] |
| LDCM0464 | CL71 | HEK-293T | C615(1.23); C601(0.88); C914(0.85); C850(0.77) | LDD1667 | [18] |
| LDCM0465 | CL72 | HEK-293T | C615(1.12); C601(1.01); C914(1.06); C850(0.98) | LDD1668 | [18] |
| LDCM0466 | CL73 | HEK-293T | C615(0.98); C601(0.94); C914(1.12); C850(1.02) | LDD1669 | [18] |
| LDCM0467 | CL74 | HEK-293T | C615(0.94); C601(0.91); C914(0.89); C850(1.07) | LDD1670 | [18] |
| LDCM0469 | CL76 | HEK-293T | C615(0.94); C601(0.91); C914(0.99); C850(1.10) | LDD1672 | [18] |
| LDCM0470 | CL77 | HEK-293T | C601(0.78); C914(0.96); C850(0.84) | LDD1673 | [18] |
| LDCM0471 | CL78 | HEK-293T | C601(0.93); C914(0.90); C850(0.96) | LDD1674 | [18] |
| LDCM0472 | CL79 | HEK-293T | C615(1.10); C601(0.90); C914(0.90); C850(1.01) | LDD1675 | [18] |
| LDCM0473 | CL8 | HEK-293T | C615(1.17); C601(0.69); C914(0.95); C850(0.87) | LDD1676 | [18] |
| LDCM0474 | CL80 | HEK-293T | C615(1.09); C601(0.95); C914(0.94); C850(1.03) | LDD1677 | [18] |
| LDCM0475 | CL81 | HEK-293T | C615(1.06); C601(1.02); C914(0.92); C850(0.95) | LDD1678 | [18] |
| LDCM0476 | CL82 | HEK-293T | C615(1.09); C601(0.94); C914(0.94); C850(0.92) | LDD1679 | [18] |
| LDCM0477 | CL83 | HEK-293T | C615(1.26); C601(0.86); C914(0.86); C850(0.94) | LDD1680 | [18] |
| LDCM0478 | CL84 | HEK-293T | C615(1.06); C601(0.97); C914(1.12); C850(0.90) | LDD1681 | [18] |
| LDCM0479 | CL85 | HEK-293T | C615(1.02); C601(0.88); C914(0.83); C850(1.07) | LDD1682 | [18] |
| LDCM0480 | CL86 | HEK-293T | C615(1.15); C601(0.84); C914(0.88); C850(1.10) | LDD1683 | [18] |
| LDCM0481 | CL87 | HEK-293T | C601(0.79); C914(0.83); C850(1.08) | LDD1684 | [18] |
| LDCM0482 | CL88 | HEK-293T | C615(0.96); C601(0.92); C914(0.92); C850(1.11) | LDD1685 | [18] |
| LDCM0483 | CL89 | HEK-293T | C601(0.81); C914(0.90); C850(0.93) | LDD1686 | [18] |
| LDCM0484 | CL9 | HEK-293T | C615(1.00); C601(0.89); C914(0.86); C850(0.97) | LDD1687 | [18] |
| LDCM0485 | CL90 | HEK-293T | C601(0.64); C914(0.80); C850(0.93) | LDD1688 | [18] |
| LDCM0486 | CL91 | HEK-293T | C615(1.03); C601(0.89); C914(0.89); C850(0.98) | LDD1689 | [18] |
| LDCM0487 | CL92 | HEK-293T | C615(1.05); C601(0.86); C914(0.99); C850(1.00) | LDD1690 | [18] |
| LDCM0488 | CL93 | HEK-293T | C615(1.15); C601(0.90); C914(0.99); C850(0.94) | LDD1691 | [18] |
| LDCM0489 | CL94 | HEK-293T | C615(1.10); C601(0.95); C914(0.90); C850(0.90) | LDD1692 | [18] |
| LDCM0490 | CL95 | HEK-293T | C615(1.38); C601(0.76); C914(1.06); C850(0.89) | LDD1693 | [18] |
| LDCM0491 | CL96 | HEK-293T | C615(1.05); C601(0.92); C914(0.96); C850(0.86) | LDD1694 | [18] |
| LDCM0492 | CL97 | HEK-293T | C615(0.75); C601(0.91); C914(0.77); C850(0.90) | LDD1695 | [18] |
| LDCM0493 | CL98 | HEK-293T | C615(0.98); C601(0.83); C914(1.04); C850(0.91) | LDD1696 | [18] |
| LDCM0494 | CL99 | HEK-293T | C601(0.85); C914(0.86); C850(1.18) | LDD1697 | [18] |
| LDCM0495 | E2913 | HEK-293T | C601(0.82); C914(0.39); C850(1.11) | LDD1698 | [18] |
| LDCM0213 | Electrophilic fragment 2 | MDA-MB-231 | C601(1.06) | LDD1702 | [7] |
| LDCM0625 | F8 | Ramos | C601(0.92) | LDD2187 | [19] |
| LDCM0572 | Fragment10 | Ramos | C601(0.73) | LDD2189 | [19] |
| LDCM0573 | Fragment11 | Ramos | C601(5.81) | LDD2190 | [19] |
| LDCM0574 | Fragment12 | Ramos | C601(0.72) | LDD2191 | [19] |
| LDCM0575 | Fragment13 | Ramos | C601(0.85) | LDD2192 | [19] |
| LDCM0576 | Fragment14 | Ramos | C601(0.87) | LDD2193 | [19] |
| LDCM0579 | Fragment20 | Ramos | C601(1.08) | LDD2194 | [19] |
| LDCM0580 | Fragment21 | Ramos | C601(0.96) | LDD2195 | [19] |
| LDCM0582 | Fragment23 | Ramos | C601(2.04) | LDD2196 | [19] |
| LDCM0578 | Fragment27 | Ramos | C601(1.06) | LDD2197 | [19] |
| LDCM0586 | Fragment28 | Ramos | C601(0.84) | LDD2198 | [19] |
| LDCM0588 | Fragment30 | Ramos | C601(0.85) | LDD2199 | [19] |
| LDCM0589 | Fragment31 | Ramos | C601(0.90) | LDD2200 | [19] |
| LDCM0590 | Fragment32 | Ramos | C601(0.80) | LDD2201 | [19] |
| LDCM0468 | Fragment33 | HEK-293T | C601(0.88); C914(0.91); C850(1.16) | LDD1671 | [18] |
| LDCM0596 | Fragment38 | Ramos | C601(0.81) | LDD2203 | [19] |
| LDCM0566 | Fragment4 | Ramos | C601(0.83) | LDD2184 | [19] |
| LDCM0427 | Fragment51 | HEK-293T | C615(0.88); C601(0.95); C914(0.65); C850(0.91) | LDD1631 | [18] |
| LDCM0610 | Fragment52 | Ramos | C601(0.78) | LDD2204 | [19] |
| LDCM0614 | Fragment56 | Ramos | C601(1.22) | LDD2205 | [19] |
| LDCM0569 | Fragment7 | Ramos | C601(0.59) | LDD2186 | [19] |
| LDCM0571 | Fragment9 | Ramos | C601(0.75) | LDD2188 | [19] |
| LDCM0116 | HHS-0101 | DM93 | Y423(0.74) | LDD0264 | [9] |
| LDCM0117 | HHS-0201 | DM93 | Y423(10.31) | LDD0265 | [9] |
| LDCM0118 | HHS-0301 | DM93 | Y423(20.00) | LDD0266 | [9] |
| LDCM0119 | HHS-0401 | DM93 | Y1007(0.81) | LDD0267 | [9] |
| LDCM0120 | HHS-0701 | DM93 | Y423(0.53); Y1007(0.57) | LDD0268 | [9] |
| LDCM0022 | KB02 | HEK-293T | C601(0.94) | LDD1492 | [18] |
| LDCM0023 | KB03 | HEK-293T | C601(0.99) | LDD1497 | [18] |
| LDCM0024 | KB05 | HMCB | C945(1.66) | LDD3312 | [6] |
| LDCM0496 | Nucleophilic fragment 11a | MDA-MB-231 | C615(0.75) | LDD2089 | [7] |
| LDCM0497 | Nucleophilic fragment 11b | MDA-MB-231 | C601(1.07) | LDD2090 | [7] |
| LDCM0500 | Nucleophilic fragment 13a | MDA-MB-231 | C615(0.99) | LDD2093 | [7] |
| LDCM0505 | Nucleophilic fragment 15b | MDA-MB-231 | C615(0.64) | LDD2098 | [7] |
| LDCM0506 | Nucleophilic fragment 16a | MDA-MB-231 | C601(0.78) | LDD2099 | [7] |
| LDCM0507 | Nucleophilic fragment 16b | MDA-MB-231 | C601(0.78) | LDD2100 | [7] |
| LDCM0511 | Nucleophilic fragment 18b | MDA-MB-231 | C601(1.06) | LDD2104 | [7] |
| LDCM0512 | Nucleophilic fragment 19a | MDA-MB-231 | C615(0.92) | LDD2105 | [7] |
| LDCM0514 | Nucleophilic fragment 20a | MDA-MB-231 | C615(1.61); C601(0.95) | LDD2107 | [7] |
| LDCM0516 | Nucleophilic fragment 21a | MDA-MB-231 | C615(0.85); C601(0.52) | LDD2109 | [7] |
| LDCM0518 | Nucleophilic fragment 22a | MDA-MB-231 | C615(1.25) | LDD2111 | [7] |
| LDCM0521 | Nucleophilic fragment 23b | MDA-MB-231 | C601(0.67) | LDD2114 | [7] |
| LDCM0526 | Nucleophilic fragment 26a | MDA-MB-231 | C615(1.80) | LDD2119 | [7] |
| LDCM0530 | Nucleophilic fragment 28a | MDA-MB-231 | C615(1.04); C601(0.86) | LDD2123 | [7] |
| LDCM0532 | Nucleophilic fragment 29a | MDA-MB-231 | C615(1.09); C601(1.31) | LDD2125 | [7] |
| LDCM0534 | Nucleophilic fragment 30a | MDA-MB-231 | C615(1.69); C601(0.95) | LDD2127 | [7] |
| LDCM0536 | Nucleophilic fragment 31 | MDA-MB-231 | C615(1.42) | LDD2129 | [7] |
| LDCM0542 | Nucleophilic fragment 37 | MDA-MB-231 | C615(1.18); C601(1.15) | LDD2135 | [7] |
| LDCM0543 | Nucleophilic fragment 38 | MDA-MB-231 | C615(1.35) | LDD2136 | [7] |
| LDCM0544 | Nucleophilic fragment 39 | MDA-MB-231 | C615(1.09); C601(0.92) | LDD2137 | [7] |
| LDCM0211 | Nucleophilic fragment 3b | MDA-MB-231 | C615(2.19) | LDD1700 | [7] |
| LDCM0546 | Nucleophilic fragment 40 | MDA-MB-231 | C615(1.26); C601(0.77) | LDD2140 | [7] |
| LDCM0547 | Nucleophilic fragment 41 | MDA-MB-231 | C601(0.68) | LDD2141 | [7] |
| LDCM0550 | Nucleophilic fragment 5a | MDA-MB-231 | C615(2.06); C601(2.95) | LDD2144 | [7] |
| LDCM0552 | Nucleophilic fragment 6a | MDA-MB-231 | C615(1.40) | LDD2146 | [7] |
| LDCM0554 | Nucleophilic fragment 7a | MDA-MB-231 | C615(0.66) | LDD2148 | [7] |
| LDCM0556 | Nucleophilic fragment 8a | MDA-MB-231 | C615(0.56) | LDD2150 | [7] |
The Interaction Atlas With This Target
References
