Details of the Target
General Information of Target
| Target ID | LDTP04116 | |||||
|---|---|---|---|---|---|---|
| Target Name | Utrophin (UTRN) | |||||
| Gene Name | UTRN | |||||
| Gene ID | 7402 | |||||
| Synonyms |
DMDL; DRP1; Utrophin; Dystrophin-related protein 1; DRP-1 |
|||||
| 3D Structure | ||||||
| Sequence |
MAKYGEHEASPDNGQNEFSDIIKSRSDEHNDVQKKTFTKWINARFSKSGKPPINDMFTDL
KDGRKLLDLLEGLTGTSLPKERGSTRVHALNNVNRVLQVLHQNNVELVNIGGTDIVDGNH KLTLGLLWSIILHWQVKDVMKDVMSDLQQTNSEKILLSWVRQTTRPYSQVNVLNFTTSWT DGLAFNAVLHRHKPDLFSWDKVVKMSPIERLEHAFSKAQTYLGIEKLLDPEDVAVQLPDK KSIIMYLTSLFEVLPQQVTIDAIREVETLPRKYKKECEEEAINIQSTAPEEEHESPRAET PSTVTEVDMDLDSYQIALEEVLTWLLSAEDTFQEQDDISDDVEEVKDQFATHEAFMMELT AHQSSVGSVLQAGNQLITQGTLSDEEEFEIQEQMTLLNARWEALRVESMDRQSRLHDVLM ELQKKQLQQLSAWLTLTEERIQKMETCPLDDDVKSLQKLLEEHKSLQSDLEAEQVKVNSL THMVVIVDENSGESATAILEDQLQKLGERWTAVCRWTEERWNRLQEINILWQELLEEQCL LKAWLTEKEEALNKVQTSNFKDQKELSVSVRRLAILKEDMEMKRQTLDQLSEIGQDVGQL LDNSKASKKINSDSEELTQRWDSLVQRLEDSSNQVTQAVAKLGMSQIPQKDLLETVRVRE QAITKKSKQELPPPPPPKKRQIHVDIEAKKKFDAISAELLNWILKWKTAIQTTEIKEYMK MQDTSEMKKKLKALEKEQRERIPRADELNQTGQILVEQMGKEGLPTEEIKNVLEKVSSEW KNVSQHLEDLERKIQLQEDINAYFKQLDELEKVIKTKEEWVKHTSISESSRQSLPSLKDS CQRELTNLLGLHPKIEMARASCSALMSQPSAPDFVQRGFDSFLGRYQAVQEAVEDRQQHL ENELKGQPGHAYLETLKTLKDVLNDSENKAQVSLNVLNDLAKVEKALQEKKTLDEILENQ KPALHKLAEETKALEKNVHPDVEKLYKQEFDDVQGKWNKLKVLVSKDLHLLEEIALTLRA FEADSTVIEKWMDGVKDFLMKQQAAQGDDAGLQRQLDQCSAFVNEIETIESSLKNMKEIE TNLRSGPVAGIKTWVQTRLGDYQTQLEKLSKEIATQKSRLSESQEKAANLKKDLAEMQEW MTQAEEEYLERDFEYKSPEELESAVEEMKRAKEDVLQKEVRVKILKDNIKLLAAKVPSGG QELTSELNVVLENYQLLCNRIRGKCHTLEEVWSCWIELLHYLDLETTWLNTLEERMKSTE VLPEKTDAVNEALESLESVLRHPADNRTQIRELGQTLIDGGILDDIISEKLEAFNSRYED LSHLAESKQISLEKQLQVLRETDQMLQVLQESLGELDKQLTTYLTDRIDAFQVPQEAQKI QAEISAHELTLEELRRNMRSQPLTSPESRTARGGSQMDVLQRKLREVSTKFQLFQKPANF EQRMLDCKRVLDGVKAELHVLDVKDVDPDVIQTHLDKCMKLYKTLSEVKLEVETVIKTGR HIVQKQQTDNPKGMDEQLTSLKVLYNDLGAQVTEGKQDLERASQLARKMKKEAASLSEWL SATETELVQKSTSEGLLGDLDTEISWAKNVLKDLEKRKADLNTITESSAALQNLIEGSEP ILEERLCVLNAGWSRVRTWTEDWCNTLMNHQNQLEIFDGNVAHISTWLYQAEALLDEIEK KPTSKQEEIVKRLVSELDDANLQVENVRDQALILMNARGSSSRELVEPKLAELNRNFEKV SQHIKSAKLLIAQEPLYQCLVTTETFETGVPFSDLEKLENDIENMLKFVEKHLESSDEDE KMDEESAQIEEVLQRGEEMLHQPMEDNKKEKIRLQLLLLHTRYNKIKAIPIQQRKMGQLA SGIRSSLLPTDYLVEINKILLCMDDVELSLNVPELNTAIYEDFSFQEDSLKNIKDQLDKL GEQIAVIHEKQPDVILEASGPEAIQIRDTLTQLNAKWDRINRMYSDRKGCFDRAMEEWRQ FHCDLNDLTQWITEAEELLVDTCAPGGSLDLEKARIHQQELEVGISSHQPSFAALNRTGD GIVQKLSQADGSFLKEKLAGLNQRWDAIVAEVKDRQPRLKGESKQVMKYRHQLDEIICWL TKAEHAMQKRSTTELGENLQELRDLTQEMEVHAEKLKWLNRTELEMLSDKSLSLPERDKI SESLRTVNMTWNKICREVPTTLKECIQEPSSVSQTRIAAHPNVQKVVLVSSASDIPVQSH RTSEISIPADLDKTITELADWLVLIDQMLKSNIVTVGDVEEINKTVSRMKITKADLEQRH PQLDYVFTLAQNLKNKASSSDMRTAITEKLERVKNQWDGTQHGVELRQQQLEDMIIDSLQ WDDHREETEELMRKYEARLYILQQARRDPLTKQISDNQILLQELGPGDGIVMAFDNVLQK LLEEYGSDDTRNVKETTEYLKTSWINLKQSIADRQNALEAEWRTVQASRRDLENFLKWIQ EAETTVNVLVDASHRENALQDSILARELKQQMQDIQAEIDAHNDIFKSIDGNRQKMVKAL GNSEEATMLQHRLDDMNQRWNDLKAKSASIRAHLEASAEKWNRLLMSLEELIKWLNMKDE ELKKQMPIGGDVPALQLQYDHCKALRRELKEKEYSVLNAVDQARVFLADQPIEAPEEPRR NLQSKTELTPEERAQKIAKAMRKQSSEVKEKWESLNAVTSNWQKQVDKALEKLRDLQGAM DDLDADMKEAESVRNGWKPVGDLLIDSLQDHIEKIMAFREEIAPINFKVKTVNDLSSQLS PLDLHPSLKMSRQLDDLNMRWKLLQVSVDDRLKQLQEAHRDFGPSSQHFLSTSVQLPWQR SISHNKVPYYINHQTQTTCWDHPKMTELFQSLADLNNVRFSAYRTAIKIRRLQKALCLDL LELSTTNEIFKQHKLNQNDQLLSVPDVINCLTTTYDGLEQMHKDLVNVPLCVDMCLNWLL NVYDTGRTGKIRVQSLKIGLMSLSKGLLEEKYRYLFKEVAGPTEMCDQRQLGLLLHDAIQ IPRQLGEVAAFGGSNIEPSVRSCFQQNNNKPEISVKEFIDWMHLEPQSMVWLPVLHRVAA AETAKHQAKCNICKECPIVGFRYRSLKHFNYDVCQSCFFSGRTAKGHKLHYPMVEYCIPT TSGEDVRDFTKVLKNKFRSKKYFAKHPRLGYLPVQTVLEGDNLETPITLISMWPEHYDPS QSPQLFHDDTHSRIEQYATRLAQMERTNGSFLTDSSSTTGSVEDEHALIQQYCQTLGGES PVSQPQSPAQILKSVEREERGELERIIADLEEEQRNLQVEYEQLKDQHLRRGLPVGSPPE SIISPHHTSEDSELIAEAKLLRQHKGRLEARMQILEDHNKQLESQLHRLRQLLEQPESDS RINGVSPWASPQHSALSYSLDPDASGPQFHQAAGEDLLAPPHDTSTDLTEVMEQIHSTFP SCCPNVPSRPQAM |
|||||
| Target Type |
Clinical trial
|
|||||
| Target Bioclass |
Enzyme
|
|||||
| Subcellular location |
Postsynaptic cell membrane
|
|||||
| Function | May play a role in anchoring the cytoskeleton to the plasma membrane. | |||||
| TTD ID | ||||||
| Uniprot ID | ||||||
| DrugMap ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
| ChEMBL ID | ||||||
Target Site Mutations in Different Cell Lines
| Cell line | Mutation details | Probe for labeling this protein in this cell | |||
|---|---|---|---|---|---|
| 22RV1 | Deletion: p.K951RfsTer32 | DBIA Probe Info | |||
| ABC1 | SNV: p.E1779K | DBIA Probe Info | |||
| AN3CA | SNV: p.A864S | DBIA Probe Info | |||
| DANG | SNV: p.V776F | DBIA Probe Info | |||
| DU145 | SNV: p.G1499R | DBIA Probe Info | |||
| FADU | SNV: p.T177S | DBIA Probe Info | |||
| HCT15 | SNV: p.L1936I; p.Y2972C | DBIA Probe Info | |||
| HKGZCC | SNV: p.N2562Y | DBIA Probe Info | |||
| HT | SNV: p.L1834S | . | |||
| HT115 | SNV: p.E737Ter; p.A3268V | DBIA Probe Info | |||
| IGROV1 | SNV: p.A1015V; p.C2839Y | DBIA Probe Info | |||
| Ishikawa (Heraklio) 02 ER | SNV: p.A372T | DBIA Probe Info | |||
| KARPAS422 | SNV: p.N2118T | . | |||
| KATOIII | SNV: p.E2156Ter | DBIA Probe Info | |||
| L428 | SNV: p.D1467Y | DBIA Probe Info | |||
| LS180 | Deletion: p.K1791NfsTer120 SNV: p.P270L |
DBIA Probe Info | |||
| LU65 | SNV: p.R3265M | DBIA Probe Info | |||
| MCC13 | SNV: p.H1982Y; p.G2946S | DBIA Probe Info | |||
| MDAMB468 | SNV: p.E212D | DBIA Probe Info | |||
| NCIH446 | SNV: p.R831L | . | |||
| NCIH716 | SNV: p.E1271K | . | |||
| P31FUJ | Deletion: p.T1288del | DBIA Probe Info | |||
| RPMI8226 | SNV: p.D2944N | DBIA Probe Info | |||
| SNU1079 | SNV: p.S19I | DBIA Probe Info | |||
| SNU478 | SNV: p.D2621Y | DBIA Probe Info | |||
| SW480 | SNV: p.T1473A | . | |||
| SW620 | SNV: p.T1473A | DBIA Probe Info | |||
| TOV21G | SNV: p.E299Ter | DBIA Probe Info | |||
| U937 | SNV: p.V3126I | DBIA Probe Info | |||
| UMUC3 | SNV: p.E2156K | DBIA Probe Info | |||
| WM1552C | SNV: p.S1795P | DBIA Probe Info | |||
Probe(s) Labeling This Target
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
|
m-APA Probe Info |
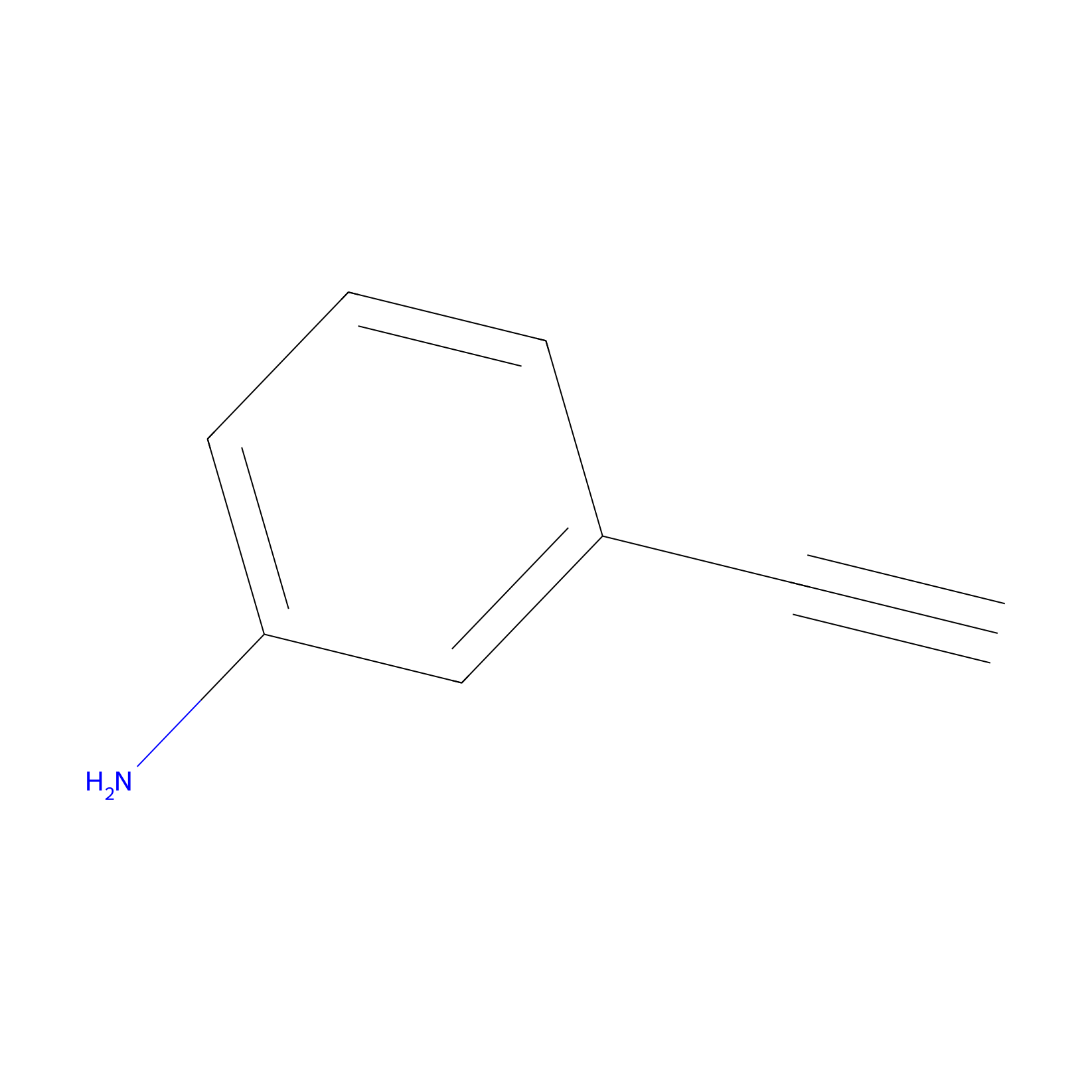 |
13.24 | LDD0402 | [1] | |
|
ONAyne Probe Info |
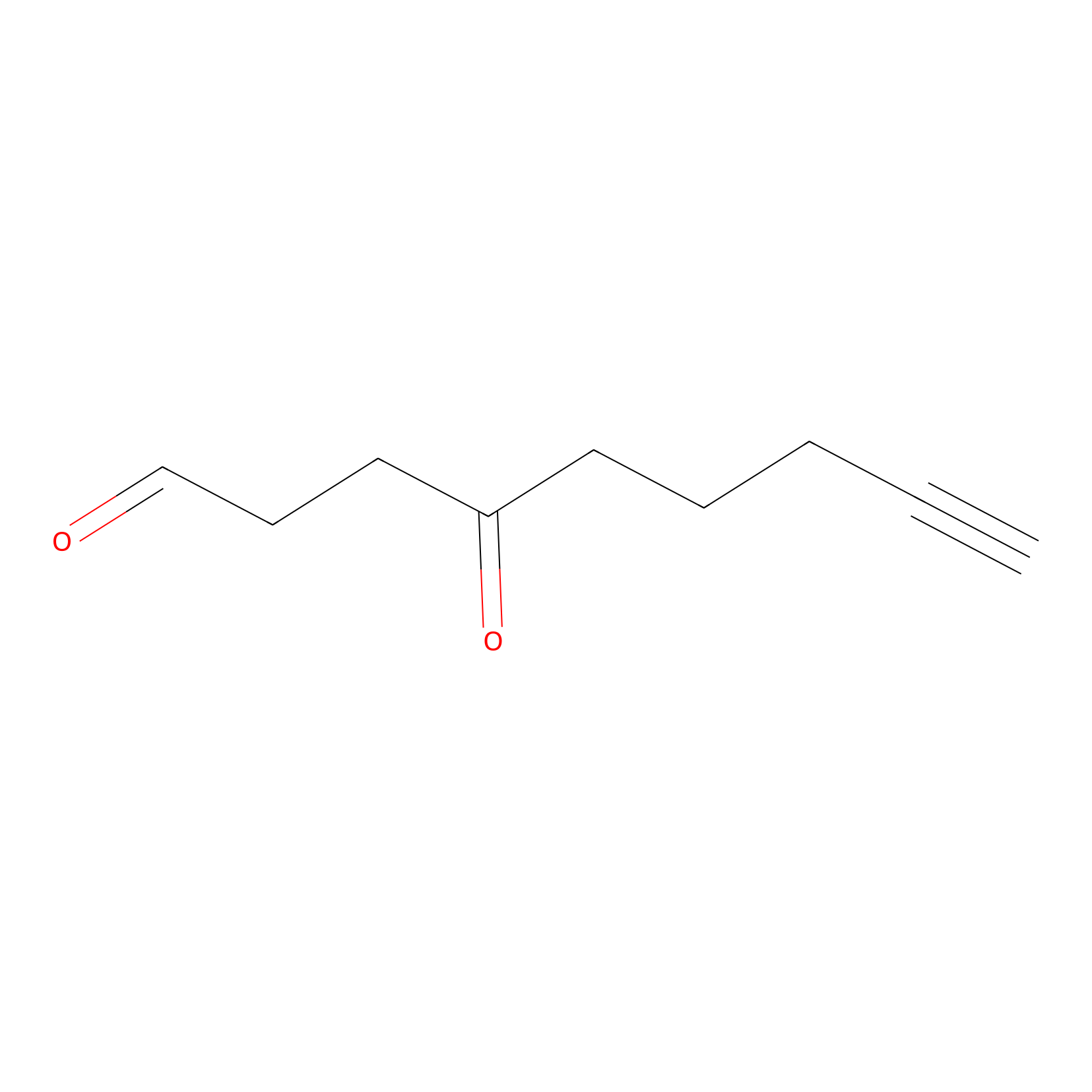 |
K2971(10.00) | LDD0275 | [2] | |
|
DBIA Probe Info |
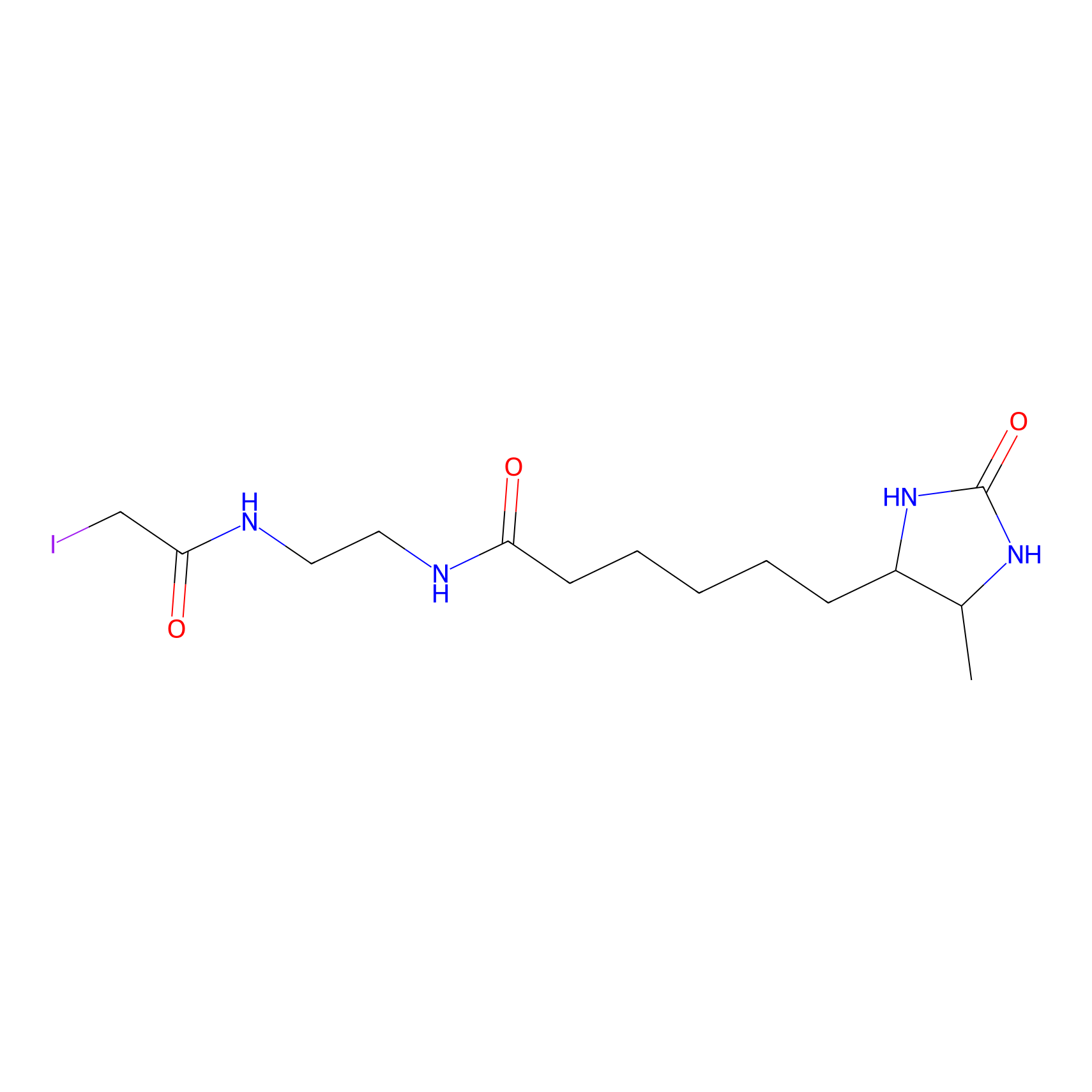 |
C99(1.69); C990(2.04); C2103(1.44) | LDD3310 | [3] | |
|
BTD Probe Info |
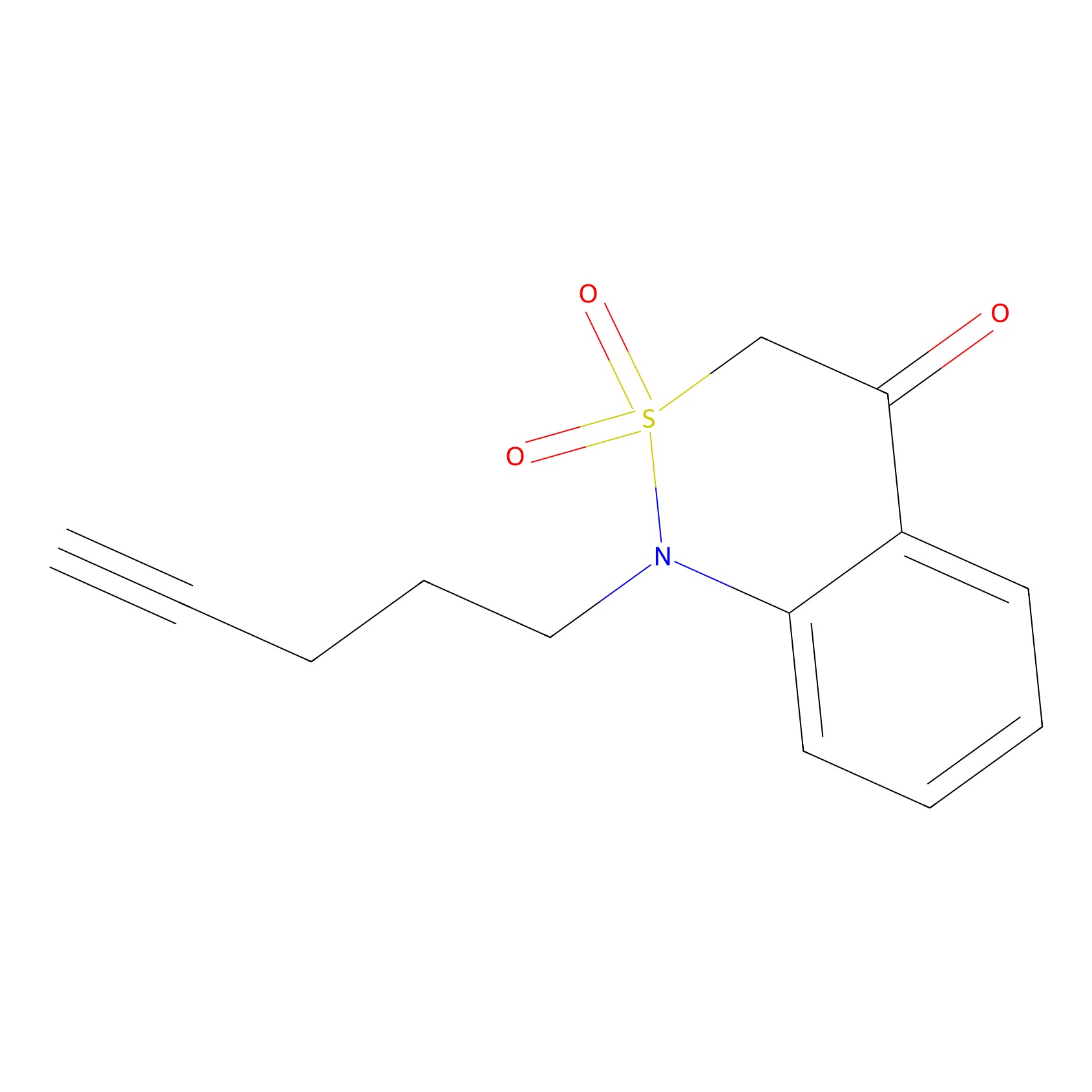 |
C3023(0.71) | LDD2089 | [4] | |
|
AHL-Pu-1 Probe Info |
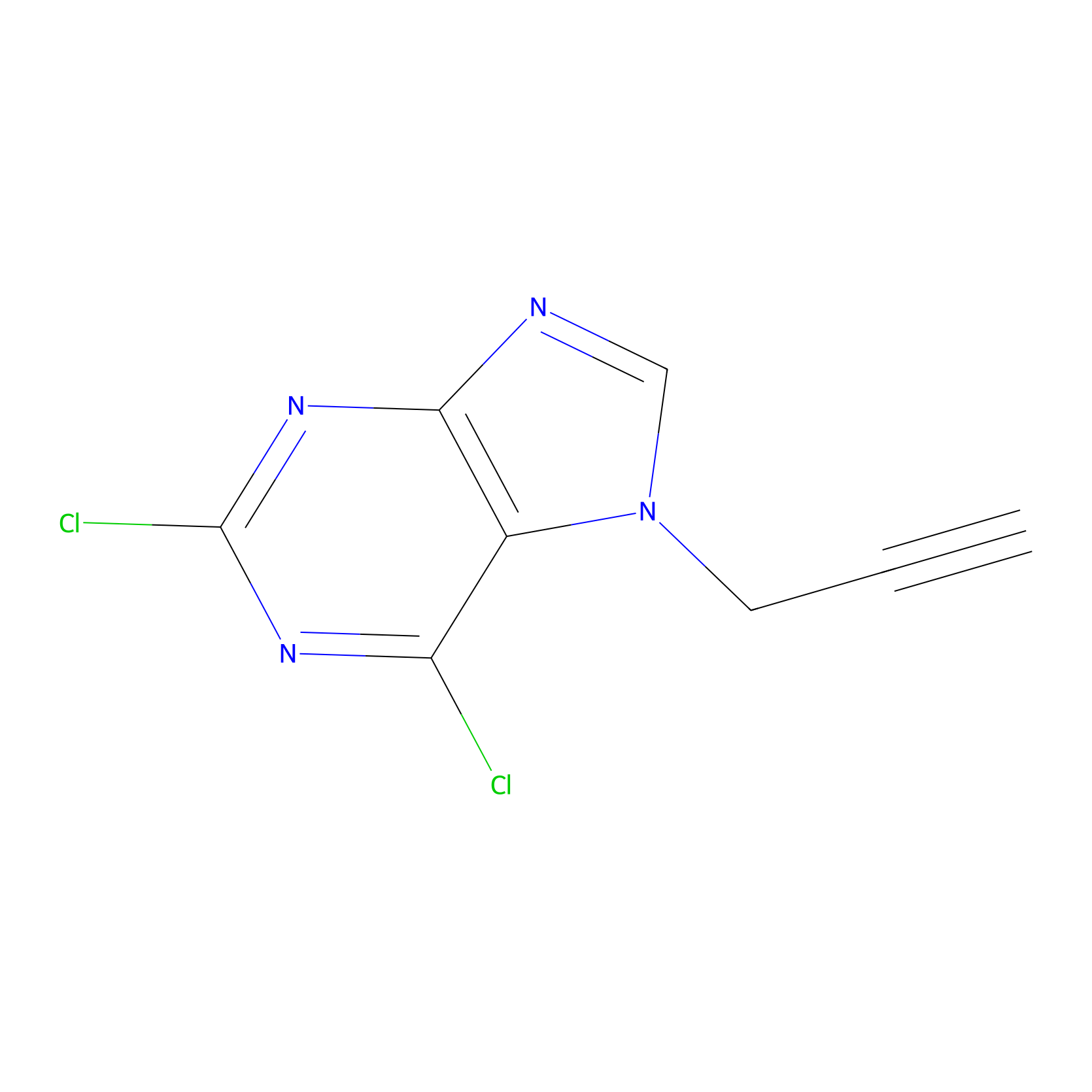 |
C539(2.60); C447(6.04) | LDD0168 | [5] | |
|
HHS-475 Probe Info |
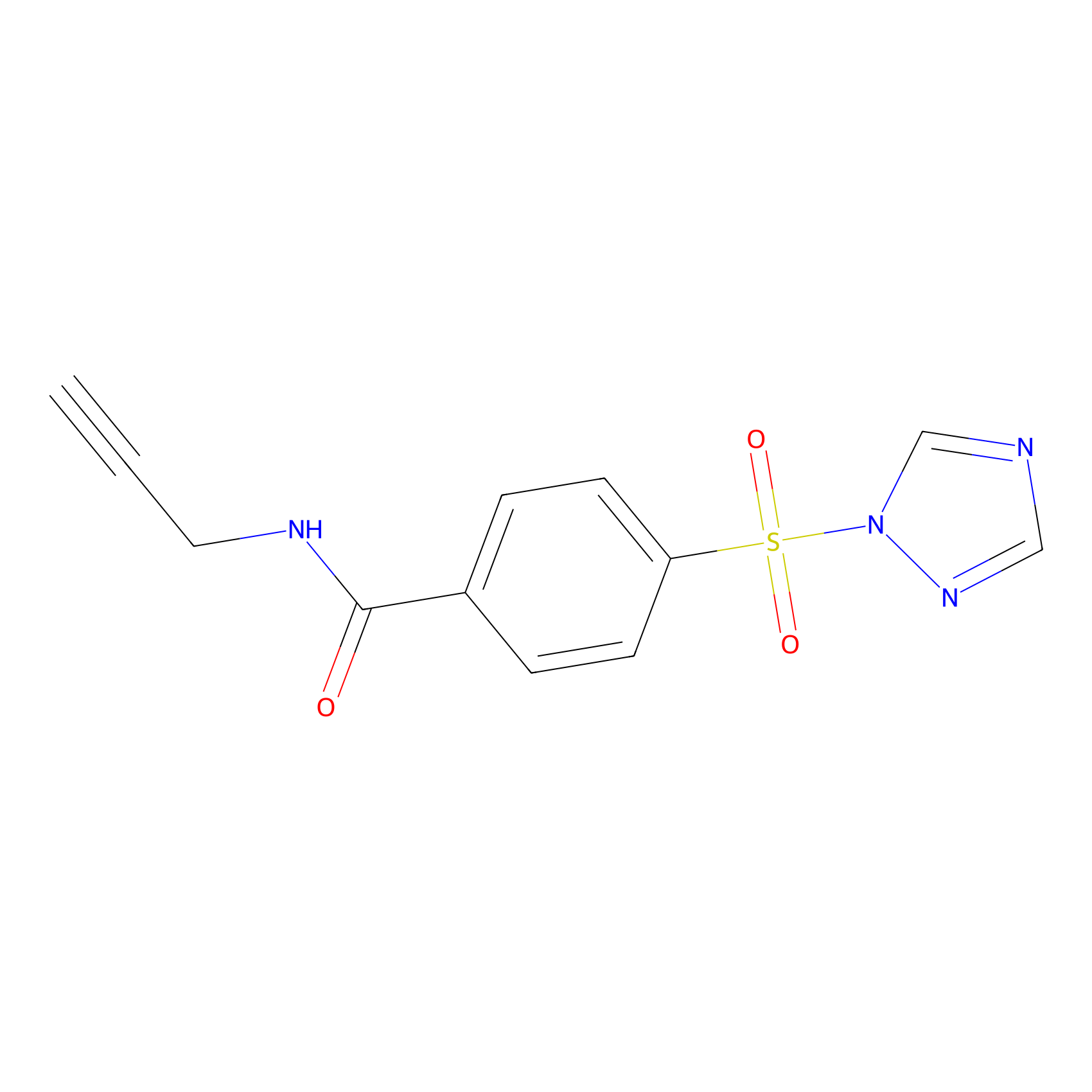 |
Y221(1.27) | LDD0264 | [6] | |
|
Acrolein Probe Info |
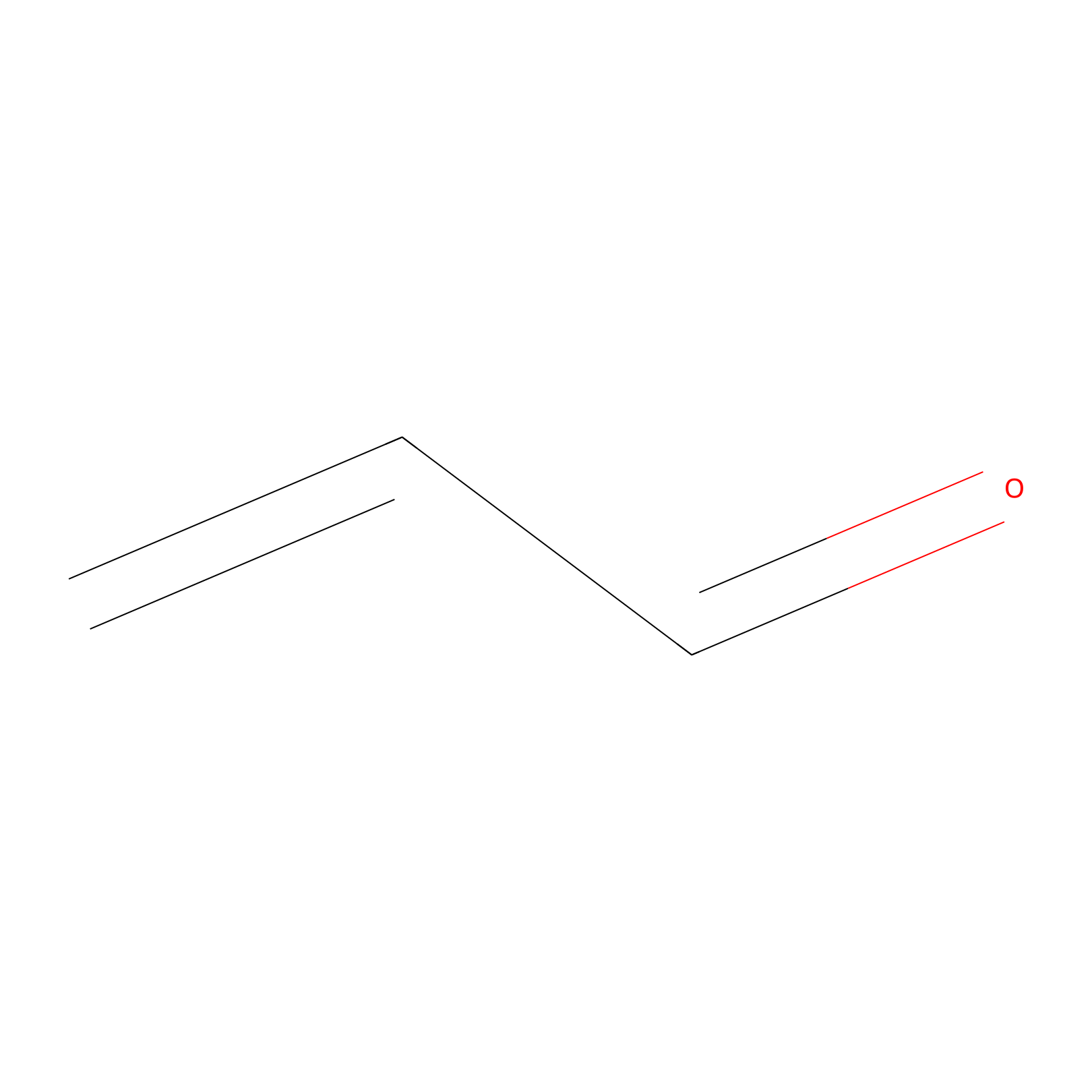 |
N.A. | LDD0223 | [7] | |
|
ATP probe Probe Info |
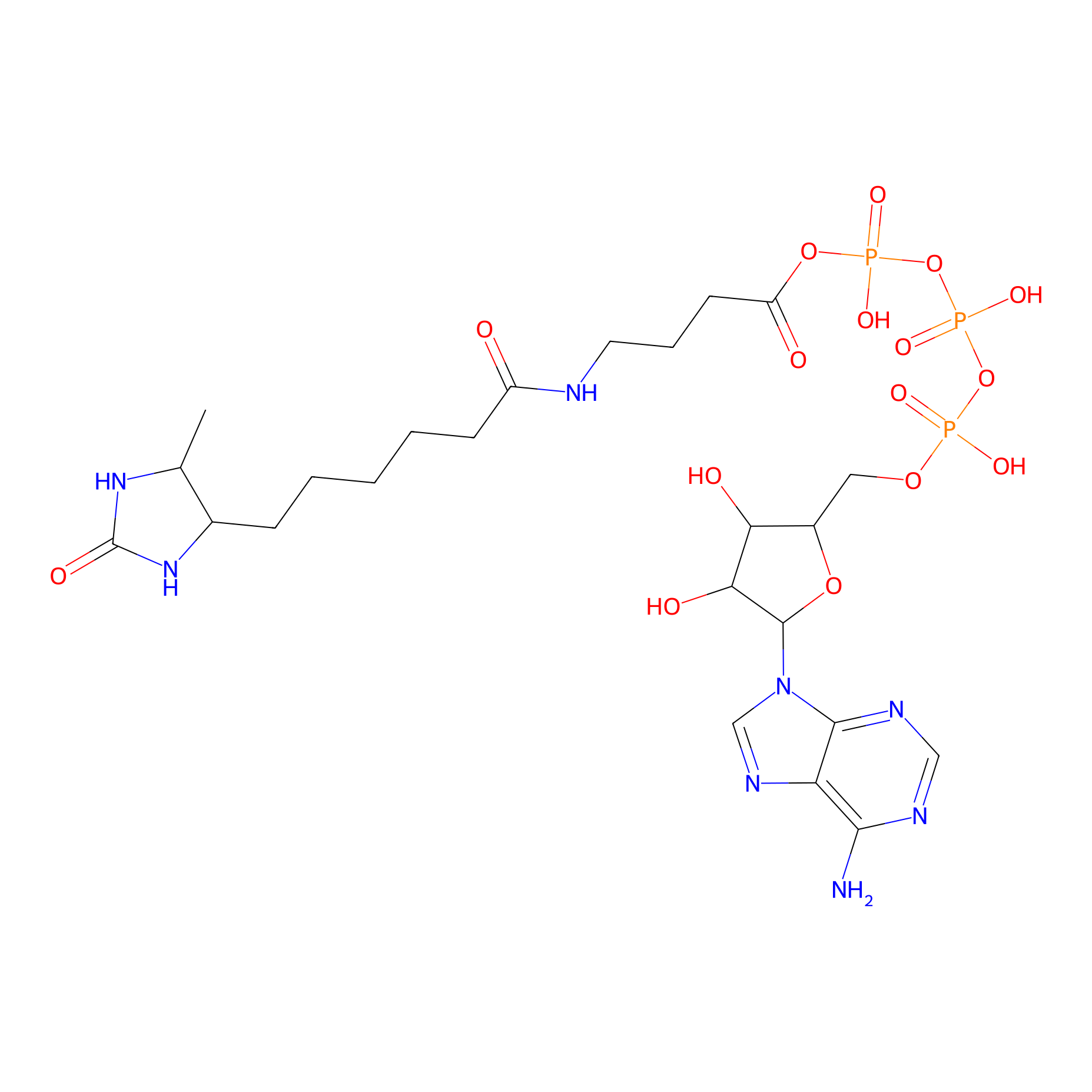 |
N.A. | LDD0199 | [8] | |
|
1d-yne Probe Info |
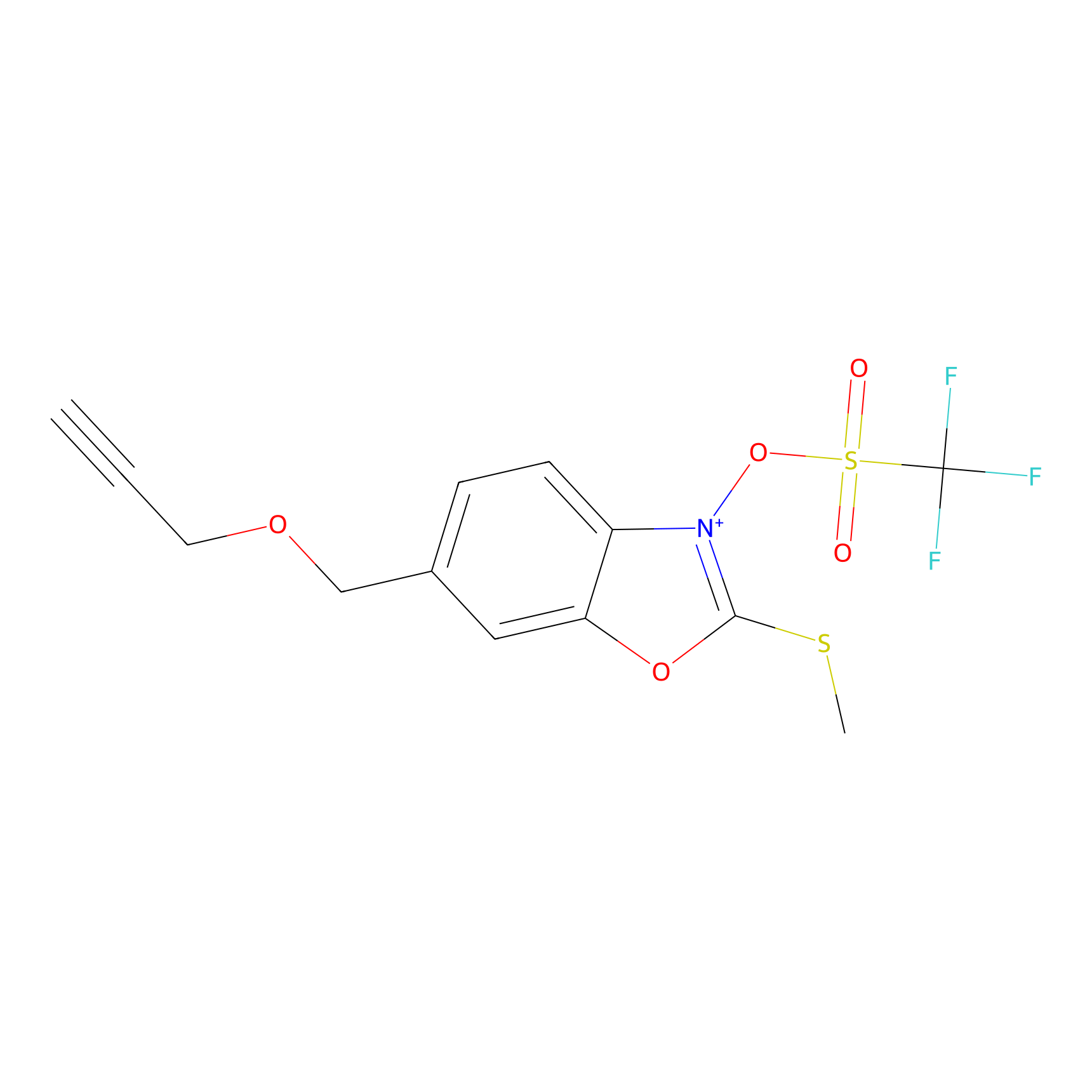 |
N.A. | LDD0358 | [9] | |
|
4-Iodoacetamidophenylacetylene Probe Info |
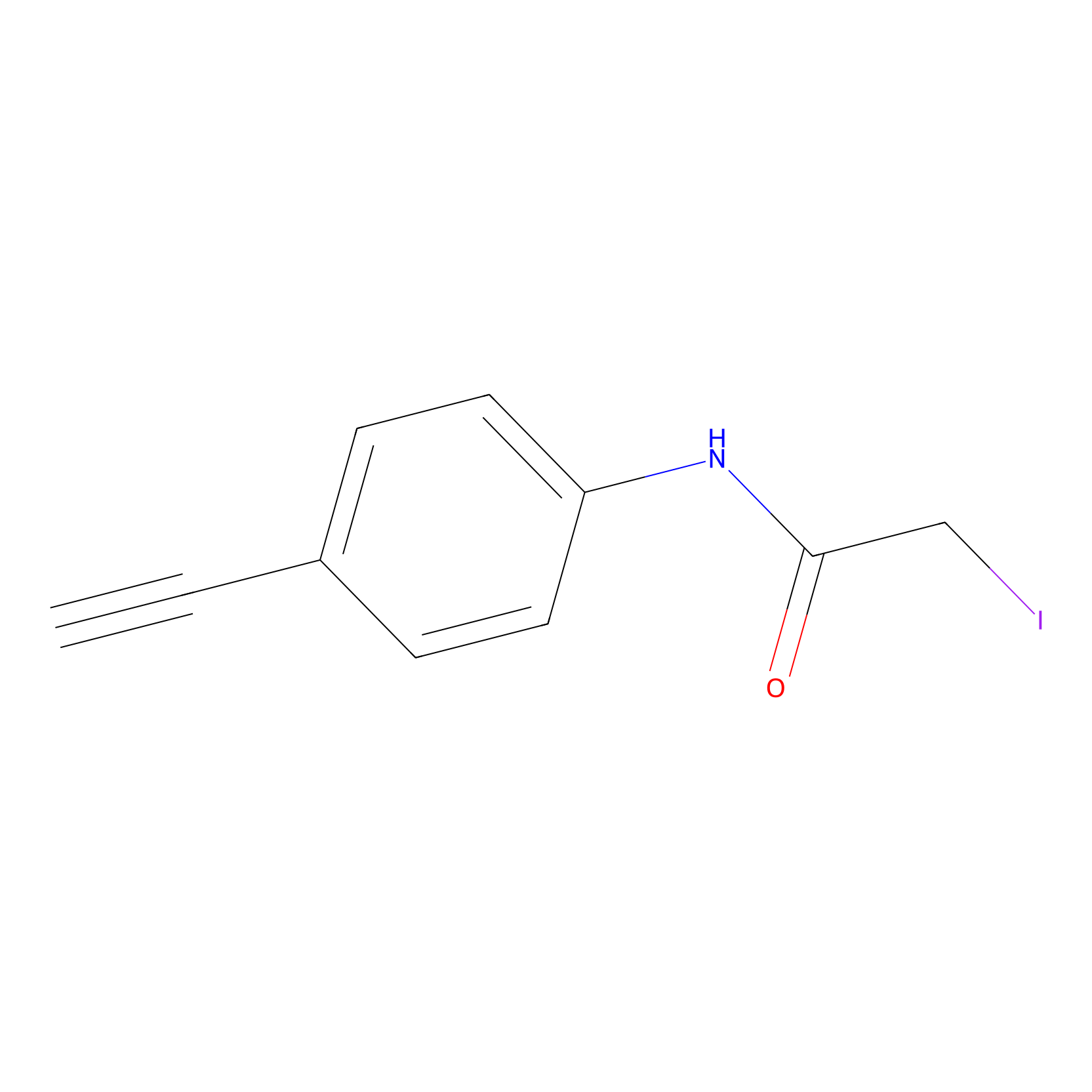 |
C2877(0.00); C1627(0.00) | LDD0038 | [10] | |
|
IA-alkyne Probe Info |
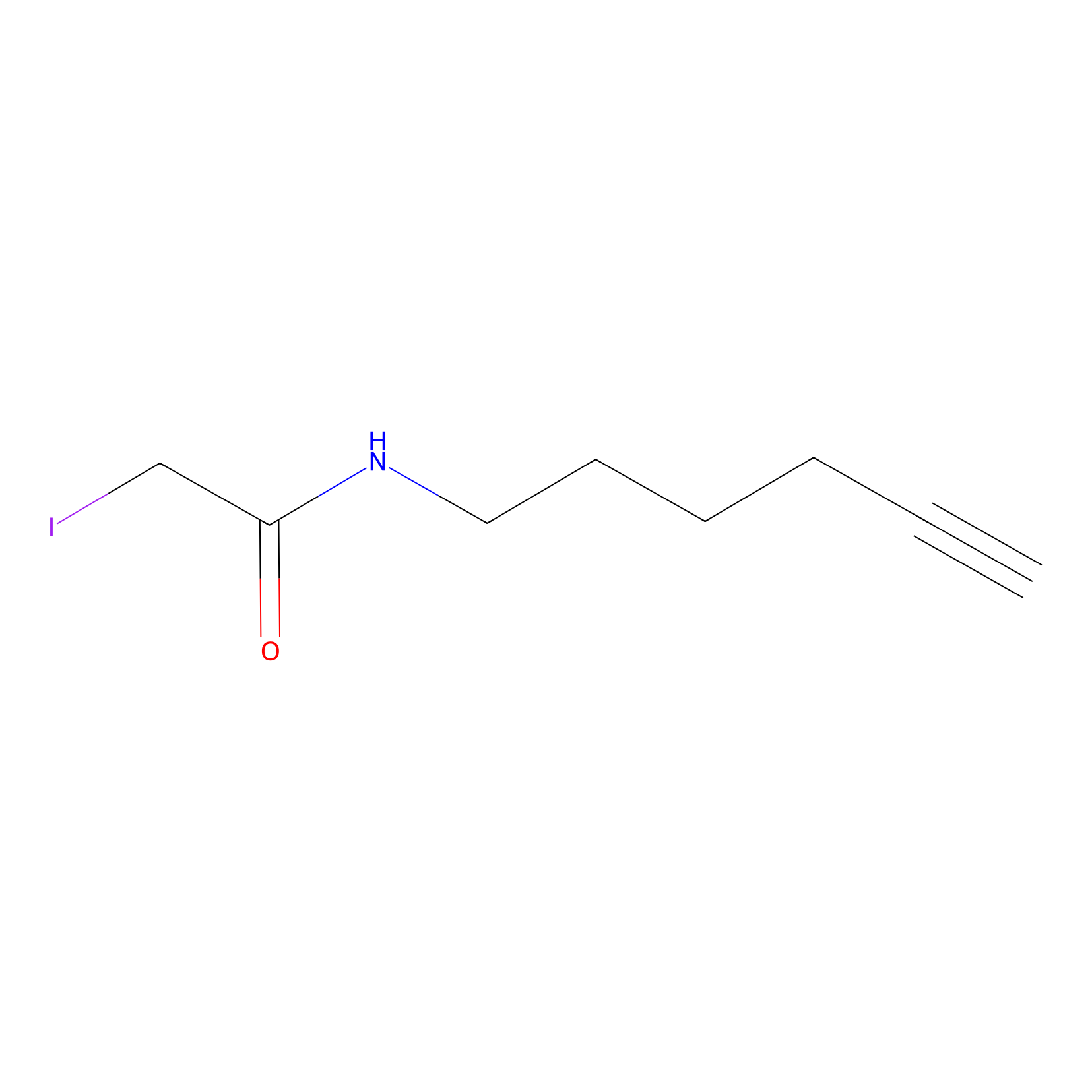 |
C3023(0.00); C2877(0.00); C1059(0.00); C1627(0.00) | LDD0036 | [10] | |
|
Lodoacetamide azide Probe Info |
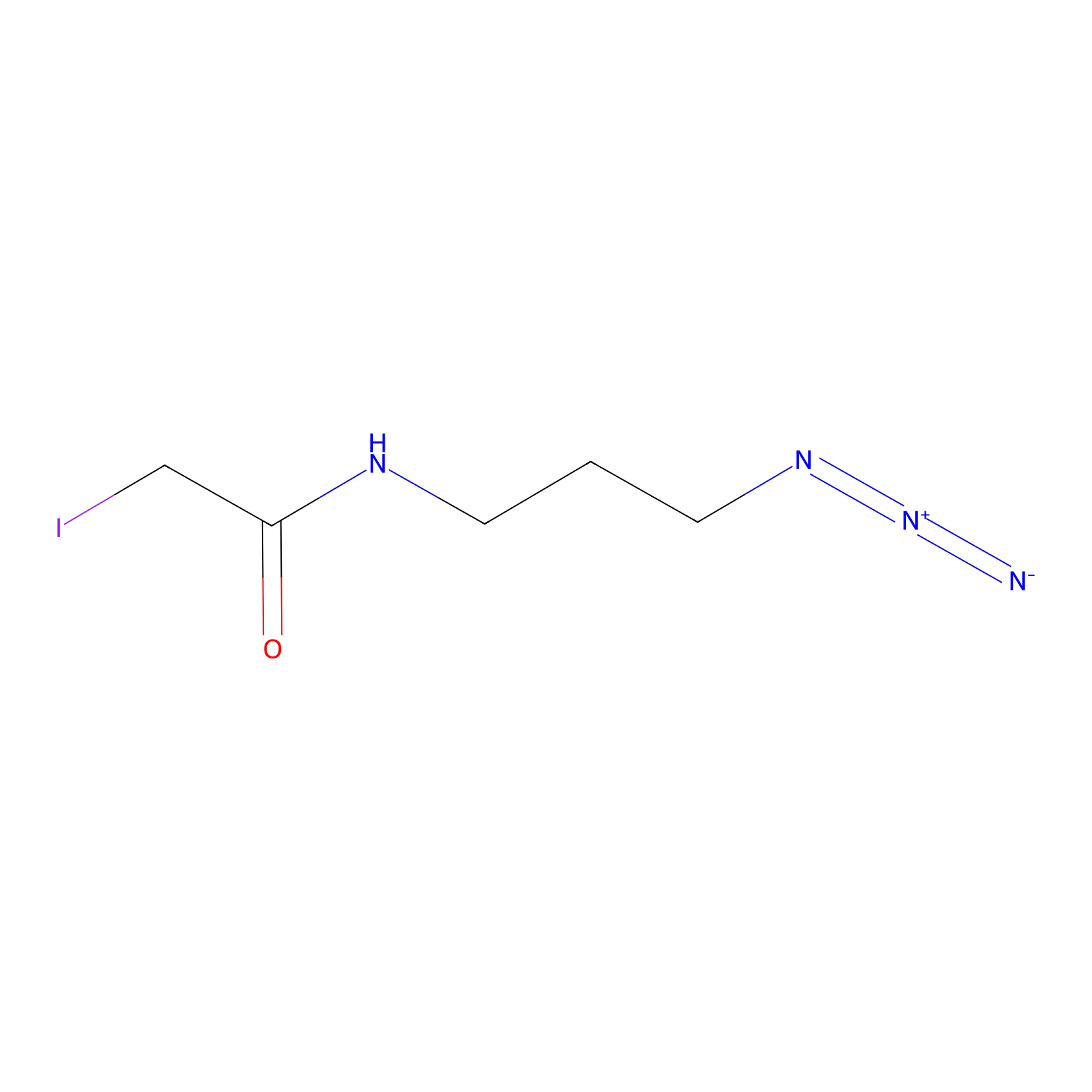 |
C3023(0.00); C1627(0.00); C1059(0.00) | LDD0037 | [10] | |
|
NAIA_4 Probe Info |
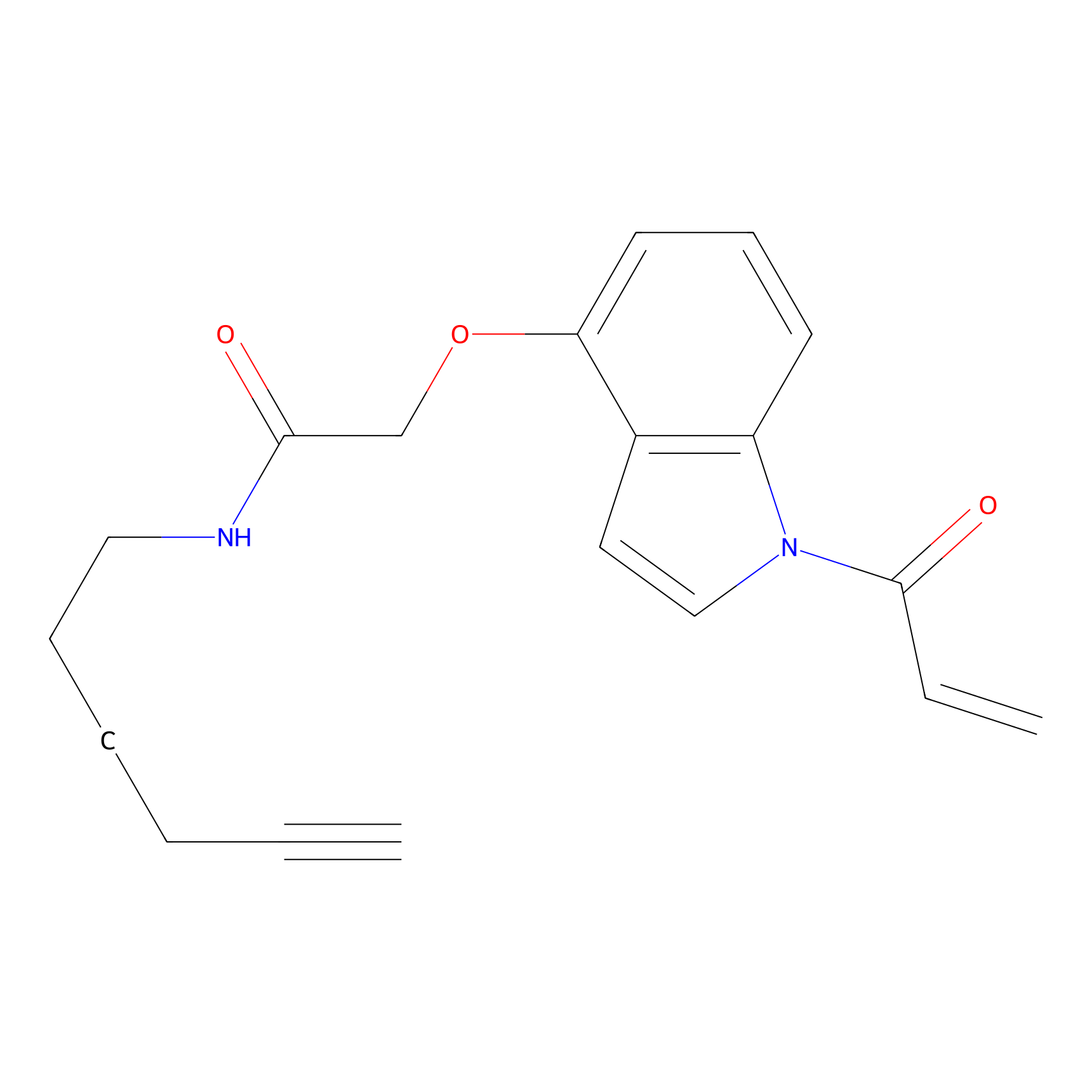 |
C2185(0.00); C2986(0.00); C3023(0.00) | LDD2226 | [11] | |
|
NAIA_5 Probe Info |
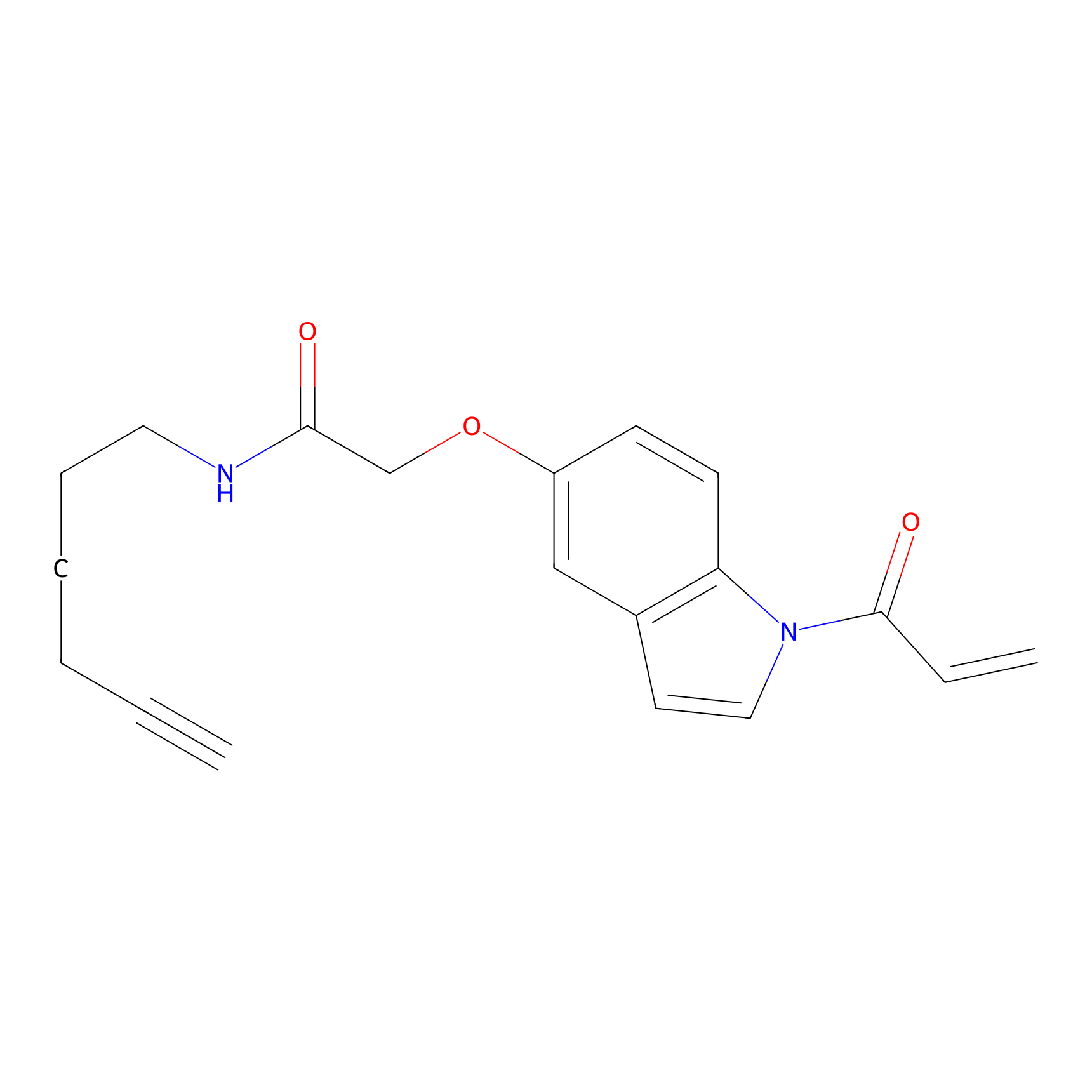 |
C2185(0.00); C2098(0.00) | LDD2224 | [11] | |
|
IPM Probe Info |
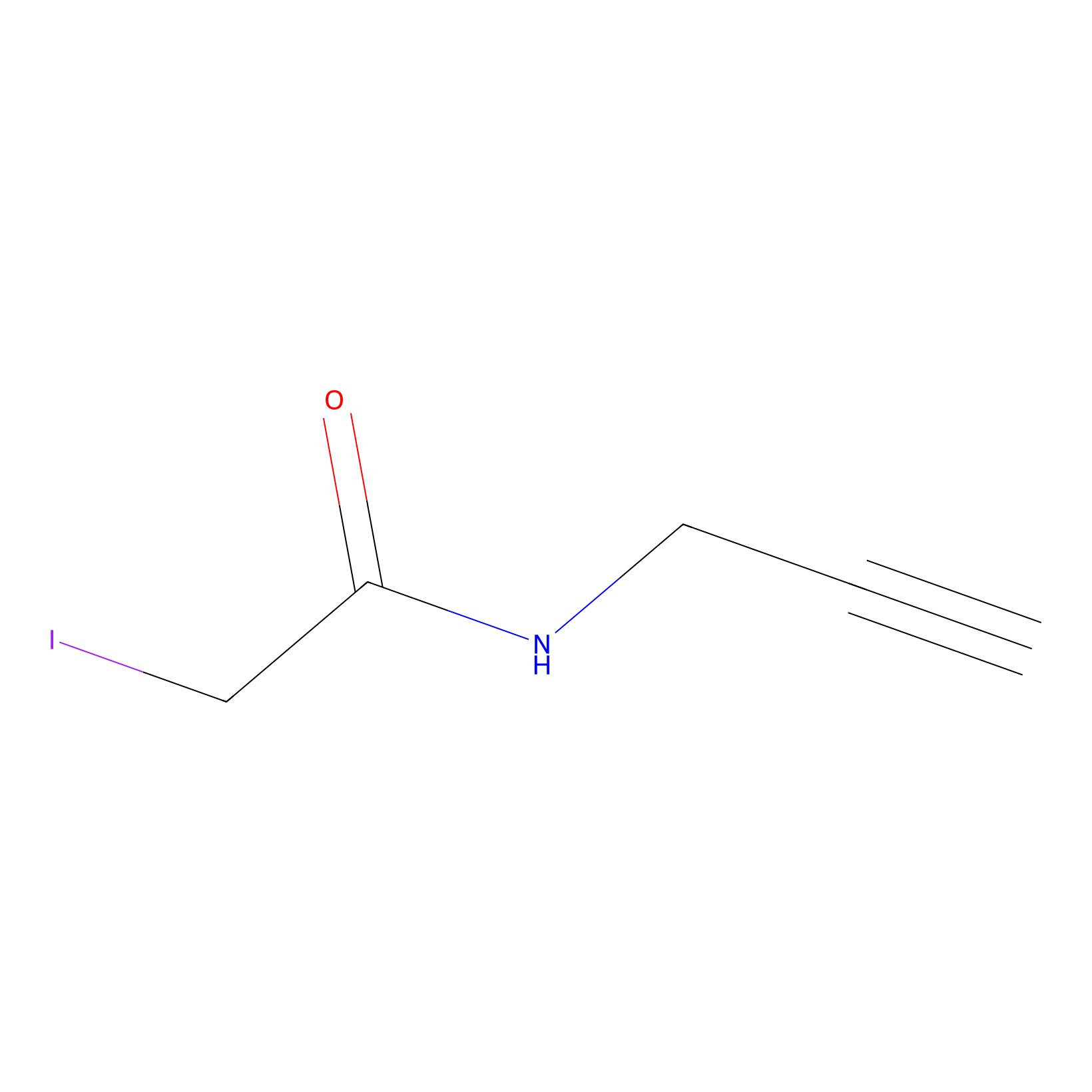 |
N.A. | LDD0005 | [12] | |
|
STPyne Probe Info |
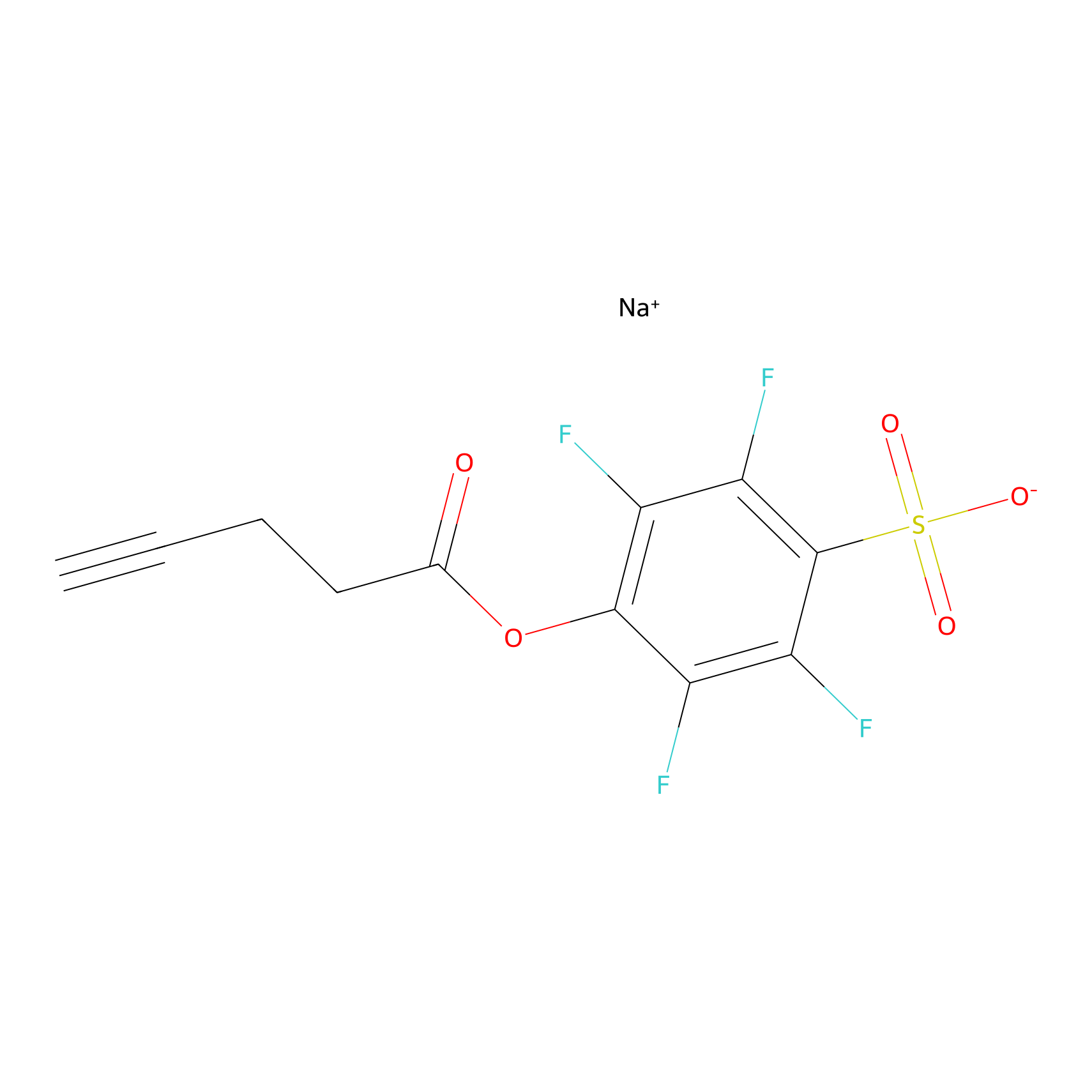 |
N.A. | LDD0009 | [12] | |
|
TFBX Probe Info |
 |
C447(0.00); C3076(0.00); C2185(0.00); C3023(0.00) | LDD0148 | [13] | |
|
VSF Probe Info |
 |
N.A. | LDD0007 | [12] | |
|
W1 Probe Info |
 |
N.A. | LDD0236 | [14] | |
|
AOyne Probe Info |
 |
9.80 | LDD0443 | [15] | |
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0502 | 1-(Cyanoacetyl)piperidine | MDA-MB-231 | C3023(0.74) | LDD2095 | [4] |
| LDCM0537 | 2-Cyano-N,N-dimethylacetamide | MDA-MB-231 | C3023(0.86) | LDD2130 | [4] |
| LDCM0524 | 2-Cyano-N-(2-morpholin-4-yl-ethyl)-acetamide | MDA-MB-231 | C1970(1.07) | LDD2117 | [4] |
| LDCM0539 | 3-(4-Isopropylpiperazin-1-yl)-3-oxopropanenitrile | MDA-MB-231 | C3023(0.56) | LDD2132 | [4] |
| LDCM0538 | 4-(Cyanoacetyl)morpholine | MDA-MB-231 | C3023(0.54) | LDD2131 | [4] |
| LDCM0025 | 4SU-RNA | HEK-293T | C539(2.60); C447(6.04) | LDD0168 | [5] |
| LDCM0026 | 4SU-RNA+native RNA | HEK-293T | C539(3.07); C447(5.70) | LDD0169 | [5] |
| LDCM0214 | AC1 | HEK-293T | C2986(1.05); C2185(0.94); C447(0.98); C3023(1.06) | LDD1507 | [16] |
| LDCM0215 | AC10 | HEK-293T | C2986(0.87); C2185(1.07); C447(0.99); C3023(0.88) | LDD1508 | [16] |
| LDCM0226 | AC11 | HEK-293T | C2986(0.90); C2185(1.03); C447(0.99); C3023(0.92) | LDD1509 | [16] |
| LDCM0237 | AC12 | HEK-293T | C2986(0.91); C2185(1.02); C447(0.98); C3023(0.90) | LDD1510 | [16] |
| LDCM0259 | AC14 | HEK-293T | C2986(0.73); C2185(1.03); C447(0.94); C3023(1.04) | LDD1512 | [16] |
| LDCM0270 | AC15 | HEK-293T | C2185(0.96); C447(1.04); C3023(1.02); C2098(1.06) | LDD1513 | [16] |
| LDCM0276 | AC17 | HEK-293T | C2986(1.39); C2185(0.93); C447(1.02); C3023(1.07) | LDD1515 | [16] |
| LDCM0277 | AC18 | HEK-293T | C2986(0.85); C2185(1.02); C447(0.97); C3023(0.91) | LDD1516 | [16] |
| LDCM0278 | AC19 | HEK-293T | C2986(1.06); C2185(0.99); C447(0.95); C3023(1.29) | LDD1517 | [16] |
| LDCM0279 | AC2 | HEK-293T | C2986(0.78); C2185(1.00); C447(1.00); C3023(0.92) | LDD1518 | [16] |
| LDCM0280 | AC20 | HEK-293T | C2986(0.89); C2185(1.12); C447(0.98); C3023(0.97) | LDD1519 | [16] |
| LDCM0281 | AC21 | HEK-293T | C2986(0.97); C2185(0.98); C447(0.99); C3023(0.99) | LDD1520 | [16] |
| LDCM0282 | AC22 | HEK-293T | C2986(0.77); C2185(0.95); C447(0.97); C3023(1.03) | LDD1521 | [16] |
| LDCM0283 | AC23 | HEK-293T | C2185(0.93); C447(0.99); C3023(1.06); C2098(0.98) | LDD1522 | [16] |
| LDCM0284 | AC24 | HEK-293T | C2986(0.92); C2185(1.01); C447(0.96); C3023(0.97) | LDD1523 | [16] |
| LDCM0285 | AC25 | HEK-293T | C2986(1.09); C2185(0.95); C447(1.01); C3023(1.07) | LDD1524 | [16] |
| LDCM0286 | AC26 | HEK-293T | C2986(0.94); C2185(1.07); C447(1.01); C3023(0.91) | LDD1525 | [16] |
| LDCM0287 | AC27 | HEK-293T | C2986(0.83); C2185(0.94); C447(1.02); C3023(0.98) | LDD1526 | [16] |
| LDCM0288 | AC28 | HEK-293T | C2986(0.92); C2185(1.13); C447(0.95); C3023(1.00) | LDD1527 | [16] |
| LDCM0289 | AC29 | HEK-293T | C2986(1.13); C2185(1.03); C447(0.96); C3023(1.00) | LDD1528 | [16] |
| LDCM0290 | AC3 | HEK-293T | C2986(0.92); C2185(0.95); C447(1.00); C3023(0.90) | LDD1529 | [16] |
| LDCM0291 | AC30 | HEK-293T | C2986(1.03); C2185(0.93); C447(0.97); C3023(1.03) | LDD1530 | [16] |
| LDCM0292 | AC31 | HEK-293T | C2185(1.02); C447(1.03); C3023(0.99); C2098(0.93) | LDD1531 | [16] |
| LDCM0293 | AC32 | HEK-293T | C2986(0.98); C2185(1.01); C447(1.00); C3023(1.01) | LDD1532 | [16] |
| LDCM0294 | AC33 | HEK-293T | C2986(0.99); C2185(1.02); C447(1.00); C3023(0.98) | LDD1533 | [16] |
| LDCM0295 | AC34 | HEK-293T | C2986(0.84); C2185(1.00); C447(0.96); C3023(0.97) | LDD1534 | [16] |
| LDCM0296 | AC35 | HEK-293T | C2986(0.95); C2185(0.94); C447(0.99); C3023(0.96) | LDD1535 | [16] |
| LDCM0297 | AC36 | HEK-293T | C2986(0.90); C2185(1.02); C447(0.96); C3023(0.93) | LDD1536 | [16] |
| LDCM0298 | AC37 | HEK-293T | C2986(1.15); C2185(0.96); C447(0.89); C3023(0.97) | LDD1537 | [16] |
| LDCM0299 | AC38 | HEK-293T | C2986(1.00); C2185(1.00); C447(0.88); C3023(0.95) | LDD1538 | [16] |
| LDCM0300 | AC39 | HEK-293T | C2185(1.00); C447(1.05); C3023(0.90); C2098(0.97) | LDD1539 | [16] |
| LDCM0301 | AC4 | HEK-293T | C2986(0.92); C2185(0.96); C447(0.96); C3023(0.93) | LDD1540 | [16] |
| LDCM0302 | AC40 | HEK-293T | C2986(0.96); C2185(0.99); C447(0.93); C3023(1.06) | LDD1541 | [16] |
| LDCM0303 | AC41 | HEK-293T | C2986(1.05); C2185(1.02); C447(1.02); C3023(1.00) | LDD1542 | [16] |
| LDCM0304 | AC42 | HEK-293T | C2986(1.07); C2185(1.15); C447(1.03); C3023(0.92) | LDD1543 | [16] |
| LDCM0305 | AC43 | HEK-293T | C2986(0.90); C2185(0.99); C447(0.95); C3023(0.92) | LDD1544 | [16] |
| LDCM0306 | AC44 | HEK-293T | C2986(0.96); C2185(1.07); C447(0.99); C3023(0.92) | LDD1545 | [16] |
| LDCM0307 | AC45 | HEK-293T | C2986(1.03); C2185(1.04); C447(0.93); C3023(0.81) | LDD1546 | [16] |
| LDCM0308 | AC46 | HEK-293T | C2986(0.88); C2185(1.00); C447(0.90); C3023(0.96) | LDD1547 | [16] |
| LDCM0309 | AC47 | HEK-293T | C2185(0.95); C447(1.01); C3023(1.01); C2098(0.88) | LDD1548 | [16] |
| LDCM0310 | AC48 | HEK-293T | C2986(0.79); C2185(1.09); C447(0.96); C3023(0.92) | LDD1549 | [16] |
| LDCM0311 | AC49 | HEK-293T | C2986(1.06); C2185(0.93); C447(1.06); C3023(0.94) | LDD1550 | [16] |
| LDCM0312 | AC5 | HEK-293T | C2986(1.08); C2185(1.01); C447(0.97); C3023(0.86) | LDD1551 | [16] |
| LDCM0313 | AC50 | HEK-293T | C2986(0.83); C2185(1.06); C447(0.99); C3023(0.93) | LDD1552 | [16] |
| LDCM0314 | AC51 | HEK-293T | C2986(0.92); C2185(0.99); C447(0.99); C3023(0.91) | LDD1553 | [16] |
| LDCM0315 | AC52 | HEK-293T | C2986(0.79); C2185(0.90); C447(0.98); C3023(0.89) | LDD1554 | [16] |
| LDCM0316 | AC53 | HEK-293T | C2986(0.99); C2185(1.01); C447(0.99); C3023(1.00) | LDD1555 | [16] |
| LDCM0317 | AC54 | HEK-293T | C2986(1.05); C2185(0.92); C447(0.97); C3023(1.01) | LDD1556 | [16] |
| LDCM0318 | AC55 | HEK-293T | C2185(0.91); C447(1.05); C3023(0.96); C2098(0.99) | LDD1557 | [16] |
| LDCM0319 | AC56 | HEK-293T | C2986(0.96); C2185(1.05); C447(0.99); C3023(0.95) | LDD1558 | [16] |
| LDCM0320 | AC57 | HEK-293T | C2986(1.39); C2185(0.97); C447(1.00); C3023(1.07) | LDD1559 | [16] |
| LDCM0321 | AC58 | HEK-293T | C2986(0.85); C2185(1.02); C447(1.01); C3023(0.96) | LDD1560 | [16] |
| LDCM0322 | AC59 | HEK-293T | C2986(0.85); C2185(0.97); C447(0.93); C3023(0.91) | LDD1561 | [16] |
| LDCM0323 | AC6 | HEK-293T | C2986(1.10); C2185(0.88); C447(0.90); C3023(1.05) | LDD1562 | [16] |
| LDCM0324 | AC60 | HEK-293T | C2986(1.22); C2185(1.00); C447(0.97); C3023(0.97) | LDD1563 | [16] |
| LDCM0325 | AC61 | HEK-293T | C2986(1.15); C2185(0.99); C447(0.96); C3023(1.00) | LDD1564 | [16] |
| LDCM0326 | AC62 | HEK-293T | C2986(0.97); C2185(0.97); C447(0.92); C3023(1.10) | LDD1565 | [16] |
| LDCM0327 | AC63 | HEK-293T | C2185(0.89); C447(0.95); C3023(1.03); C2098(1.01) | LDD1566 | [16] |
| LDCM0328 | AC64 | HEK-293T | C2986(0.82); C2185(0.96); C447(0.92); C3023(0.96) | LDD1567 | [16] |
| LDCM0334 | AC7 | HEK-293T | C2185(1.03); C447(1.01); C3023(0.98); C2098(1.03) | LDD1568 | [16] |
| LDCM0345 | AC8 | HEK-293T | C2986(0.86); C2185(1.04); C447(0.94); C3023(1.00) | LDD1569 | [16] |
| LDCM0545 | Acetamide | MDA-MB-231 | C3023(0.59); C1970(1.46) | LDD2138 | [4] |
| LDCM0248 | AKOS034007472 | HEK-293T | C2986(1.10); C2185(1.01); C447(1.02); C3023(0.97) | LDD1511 | [16] |
| LDCM0356 | AKOS034007680 | HEK-293T | C2986(0.86); C2185(1.13); C447(1.06); C3023(1.12) | LDD1570 | [16] |
| LDCM0275 | AKOS034007705 | HEK-293T | C2986(1.11); C2185(1.04); C447(1.00); C3023(1.00) | LDD1514 | [16] |
| LDCM0156 | Aniline | NCI-H1299 | N.A. | LDD0404 | [1] |
| LDCM0498 | BS-3668 | MDA-MB-231 | C3023(0.74) | LDD2091 | [4] |
| LDCM0632 | CL-Sc | Hep-G2 | C2098(0.81) | LDD2227 | [11] |
| LDCM0367 | CL1 | HEK-293T | C2986(0.85); C2185(0.94); C447(0.98); C3023(1.00) | LDD1571 | [16] |
| LDCM0368 | CL10 | HEK-293T | C2986(1.22); C2185(0.85); C447(1.03); C3023(1.22) | LDD1572 | [16] |
| LDCM0369 | CL100 | HEK-293T | C2986(0.97); C2185(1.01); C447(0.96); C3023(1.13) | LDD1573 | [16] |
| LDCM0370 | CL101 | HEK-293T | C2986(0.71); C2185(0.87); C447(1.03); C3023(1.01) | LDD1574 | [16] |
| LDCM0371 | CL102 | HEK-293T | C2986(1.39); C2185(0.90); C447(1.12); C3023(1.02) | LDD1575 | [16] |
| LDCM0372 | CL103 | HEK-293T | C2986(0.93); C2185(0.88); C447(0.95); C3023(1.05) | LDD1576 | [16] |
| LDCM0373 | CL104 | HEK-293T | C2986(1.06); C2185(0.92); C447(0.96); C3023(0.89) | LDD1577 | [16] |
| LDCM0374 | CL105 | HEK-293T | C2986(0.62); C2185(0.89); C447(1.00); C3023(1.03) | LDD1578 | [16] |
| LDCM0375 | CL106 | HEK-293T | C2986(1.20); C2185(0.87); C447(1.01); C3023(0.92) | LDD1579 | [16] |
| LDCM0376 | CL107 | HEK-293T | C2986(1.21); C2185(0.92); C447(0.94); C3023(0.98) | LDD1580 | [16] |
| LDCM0377 | CL108 | HEK-293T | C2986(0.94); C2185(1.14); C447(1.03); C3023(0.90) | LDD1581 | [16] |
| LDCM0378 | CL109 | HEK-293T | C2986(0.76); C2185(0.93); C447(1.01); C3023(1.03) | LDD1582 | [16] |
| LDCM0379 | CL11 | HEK-293T | C2185(1.00); C447(1.03); C3023(0.84); C2098(0.98) | LDD1583 | [16] |
| LDCM0380 | CL110 | HEK-293T | C2986(1.25); C2185(0.87); C447(1.07); C3023(1.09) | LDD1584 | [16] |
| LDCM0381 | CL111 | HEK-293T | C2986(0.96); C2185(0.88); C447(0.90); C3023(1.08) | LDD1585 | [16] |
| LDCM0382 | CL112 | HEK-293T | C2986(0.89); C2185(0.87); C447(1.06); C3023(0.92) | LDD1586 | [16] |
| LDCM0383 | CL113 | HEK-293T | C2986(0.70); C2185(0.89); C447(0.97); C3023(0.97) | LDD1587 | [16] |
| LDCM0384 | CL114 | HEK-293T | C2986(1.05); C2185(0.84); C447(1.38); C3023(1.09) | LDD1588 | [16] |
| LDCM0385 | CL115 | HEK-293T | C2986(0.78); C2185(0.99); C447(1.03); C3023(0.97) | LDD1589 | [16] |
| LDCM0386 | CL116 | HEK-293T | C2986(1.03); C2185(0.95); C447(1.03); C3023(0.97) | LDD1590 | [16] |
| LDCM0387 | CL117 | HEK-293T | C2986(0.75); C2185(0.93); C447(0.95); C3023(0.92) | LDD1591 | [16] |
| LDCM0388 | CL118 | HEK-293T | C2986(1.13); C2185(0.87); C447(0.95); C3023(0.96) | LDD1592 | [16] |
| LDCM0389 | CL119 | HEK-293T | C2986(1.02); C2185(0.89); C447(0.95); C3023(0.97) | LDD1593 | [16] |
| LDCM0390 | CL12 | HEK-293T | C2986(1.03); C2185(1.14); C447(1.02); C3023(0.99) | LDD1594 | [16] |
| LDCM0391 | CL120 | HEK-293T | C2986(0.99); C2185(1.04); C447(0.97); C3023(0.91) | LDD1595 | [16] |
| LDCM0392 | CL121 | HEK-293T | C2986(0.77); C2185(1.03); C447(0.97); C3023(0.94) | LDD1596 | [16] |
| LDCM0393 | CL122 | HEK-293T | C2986(1.34); C2185(1.01); C447(1.00); C3023(0.96) | LDD1597 | [16] |
| LDCM0394 | CL123 | HEK-293T | C2986(1.51); C2185(0.87); C447(0.92); C3023(0.98) | LDD1598 | [16] |
| LDCM0395 | CL124 | HEK-293T | C2986(0.89); C2185(0.98); C447(1.08); C3023(0.96) | LDD1599 | [16] |
| LDCM0396 | CL125 | HEK-293T | C2986(0.81); C2185(0.91); C447(0.93); C3023(0.96) | LDD1600 | [16] |
| LDCM0397 | CL126 | HEK-293T | C2986(1.09); C2185(0.98); C447(0.97); C3023(1.00) | LDD1601 | [16] |
| LDCM0398 | CL127 | HEK-293T | C2986(0.81); C2185(0.92); C447(0.93); C3023(0.92) | LDD1602 | [16] |
| LDCM0399 | CL128 | HEK-293T | C2986(0.86); C2185(1.01); C447(0.96); C3023(1.00) | LDD1603 | [16] |
| LDCM0400 | CL13 | HEK-293T | C2986(0.65); C2185(1.02); C447(0.98); C3023(1.01) | LDD1604 | [16] |
| LDCM0401 | CL14 | HEK-293T | C2986(1.25); C2185(0.91); C447(1.04); C3023(0.88) | LDD1605 | [16] |
| LDCM0402 | CL15 | HEK-293T | C2986(1.07); C2185(0.75); C447(0.82); C3023(1.09) | LDD1606 | [16] |
| LDCM0403 | CL16 | HEK-293T | C2986(0.96); C2185(1.17); C447(1.03); C3023(0.98) | LDD1607 | [16] |
| LDCM0404 | CL17 | HEK-293T | C2986(1.12); C2185(0.83); C447(0.97); C3023(1.19) | LDD1608 | [16] |
| LDCM0405 | CL18 | HEK-293T | C2986(0.95); C2185(1.03); C447(1.06); C3023(0.94) | LDD1609 | [16] |
| LDCM0406 | CL19 | HEK-293T | C2986(0.89); C2185(0.97); C447(1.09); C3023(0.95) | LDD1610 | [16] |
| LDCM0407 | CL2 | HEK-293T | C2986(1.06); C2185(0.87); C447(1.00); C3023(0.83) | LDD1611 | [16] |
| LDCM0408 | CL20 | HEK-293T | C2986(0.90); C2185(1.10); C447(0.96); C3023(0.90) | LDD1612 | [16] |
| LDCM0409 | CL21 | HEK-293T | C2986(1.26); C2185(0.93); C447(1.04); C3023(1.22) | LDD1613 | [16] |
| LDCM0410 | CL22 | HEK-293T | C2986(1.07); C2185(1.01); C447(1.13); C3023(0.96) | LDD1614 | [16] |
| LDCM0411 | CL23 | HEK-293T | C2185(0.99); C447(1.11); C3023(0.86); C2098(0.98) | LDD1615 | [16] |
| LDCM0412 | CL24 | HEK-293T | C2986(0.85); C2185(1.08); C447(1.06); C3023(0.92) | LDD1616 | [16] |
| LDCM0413 | CL25 | HEK-293T | C2986(0.82); C2185(0.81); C447(0.89); C3023(1.07) | LDD1617 | [16] |
| LDCM0414 | CL26 | HEK-293T | C2986(1.36); C2185(0.86); C447(0.96); C3023(0.93) | LDD1618 | [16] |
| LDCM0415 | CL27 | HEK-293T | C2986(1.02); C2185(1.00); C447(0.97); C3023(1.01) | LDD1619 | [16] |
| LDCM0416 | CL28 | HEK-293T | C2986(0.97); C2185(1.14); C447(1.06); C3023(1.01) | LDD1620 | [16] |
| LDCM0417 | CL29 | HEK-293T | C2986(0.89); C2185(1.01); C447(1.02); C3023(0.98) | LDD1621 | [16] |
| LDCM0418 | CL3 | HEK-293T | C2986(1.05); C2185(0.83); C447(0.93); C3023(0.96) | LDD1622 | [16] |
| LDCM0419 | CL30 | HEK-293T | C2986(0.84); C2185(0.92); C447(1.02); C3023(0.92) | LDD1623 | [16] |
| LDCM0420 | CL31 | HEK-293T | C2986(0.85); C2185(1.03); C447(1.09); C3023(0.94) | LDD1624 | [16] |
| LDCM0421 | CL32 | HEK-293T | C2986(1.11); C2185(0.98); C447(1.03); C3023(0.86) | LDD1625 | [16] |
| LDCM0422 | CL33 | HEK-293T | C2986(1.97); C2185(0.89); C447(0.92); C3023(1.20) | LDD1626 | [16] |
| LDCM0423 | CL34 | HEK-293T | C2986(1.18); C2185(0.91); C447(1.07); C3023(0.95) | LDD1627 | [16] |
| LDCM0424 | CL35 | HEK-293T | C2185(1.08); C447(1.04); C3023(0.95); C2098(1.19) | LDD1628 | [16] |
| LDCM0425 | CL36 | HEK-293T | C2986(1.17); C2185(0.96); C447(1.06); C3023(0.88) | LDD1629 | [16] |
| LDCM0426 | CL37 | HEK-293T | C2986(0.85); C2185(0.92); C447(0.94); C3023(0.99) | LDD1630 | [16] |
| LDCM0428 | CL39 | HEK-293T | C2986(1.12); C2185(0.95); C447(0.94); C3023(1.04) | LDD1632 | [16] |
| LDCM0429 | CL4 | HEK-293T | C2986(1.10); C2185(1.04); C447(1.02); C3023(0.89) | LDD1633 | [16] |
| LDCM0430 | CL40 | HEK-293T | C2986(1.07); C2185(0.97); C447(1.09); C3023(0.95) | LDD1634 | [16] |
| LDCM0431 | CL41 | HEK-293T | C2986(1.09); C2185(1.00); C447(0.98); C3023(1.14) | LDD1635 | [16] |
| LDCM0432 | CL42 | HEK-293T | C2986(1.02); C2185(1.00); C447(1.07); C3023(0.89) | LDD1636 | [16] |
| LDCM0433 | CL43 | HEK-293T | C2986(1.06); C2185(0.94); C447(1.00); C3023(0.86) | LDD1637 | [16] |
| LDCM0434 | CL44 | HEK-293T | C2986(0.96); C2185(0.94); C447(1.04); C3023(0.85) | LDD1638 | [16] |
| LDCM0435 | CL45 | HEK-293T | C2986(1.12); C2185(1.10); C447(1.01); C3023(0.99) | LDD1639 | [16] |
| LDCM0436 | CL46 | HEK-293T | C2986(0.90); C2185(0.99); C447(1.15); C3023(0.89) | LDD1640 | [16] |
| LDCM0437 | CL47 | HEK-293T | C2185(0.94); C447(1.04); C3023(0.99); C2098(1.02) | LDD1641 | [16] |
| LDCM0438 | CL48 | HEK-293T | C2986(0.93); C2185(1.05); C447(1.08); C3023(0.90) | LDD1642 | [16] |
| LDCM0439 | CL49 | HEK-293T | C2986(0.64); C2185(0.82); C447(0.91); C3023(0.93) | LDD1643 | [16] |
| LDCM0440 | CL5 | HEK-293T | C2986(0.94); C2185(0.93); C447(1.02); C3023(0.95) | LDD1644 | [16] |
| LDCM0441 | CL50 | HEK-293T | C2986(1.10); C2185(0.84); C447(1.12); C3023(1.03) | LDD1645 | [16] |
| LDCM0443 | CL52 | HEK-293T | C2986(0.81); C2185(1.00); C447(1.00); C3023(0.88) | LDD1646 | [16] |
| LDCM0444 | CL53 | HEK-293T | C2986(1.16); C2185(0.94); C447(0.99); C3023(1.08) | LDD1647 | [16] |
| LDCM0445 | CL54 | HEK-293T | C2986(1.02); C2185(0.97); C447(1.10); C3023(0.89) | LDD1648 | [16] |
| LDCM0446 | CL55 | HEK-293T | C2986(0.76); C2185(1.03); C447(1.03); C3023(0.90) | LDD1649 | [16] |
| LDCM0447 | CL56 | HEK-293T | C2986(0.84); C2185(1.01); C447(0.99); C3023(0.84) | LDD1650 | [16] |
| LDCM0448 | CL57 | HEK-293T | C2986(1.52); C2185(0.94); C447(0.91); C3023(1.19) | LDD1651 | [16] |
| LDCM0449 | CL58 | HEK-293T | C2986(0.94); C2185(0.89); C447(1.09); C3023(0.91) | LDD1652 | [16] |
| LDCM0450 | CL59 | HEK-293T | C2185(0.99); C447(1.04); C3023(0.89); C2098(0.97) | LDD1653 | [16] |
| LDCM0451 | CL6 | HEK-293T | C2986(0.99); C2185(0.98); C447(1.22); C3023(1.05) | LDD1654 | [16] |
| LDCM0452 | CL60 | HEK-293T | C2986(0.81); C2185(1.09); C447(1.03); C3023(0.84) | LDD1655 | [16] |
| LDCM0453 | CL61 | HEK-293T | C2986(0.54); C2185(1.07); C447(0.98); C3023(0.90) | LDD1656 | [16] |
| LDCM0454 | CL62 | HEK-293T | C2986(0.95); C2185(1.00); C447(0.98); C3023(0.87) | LDD1657 | [16] |
| LDCM0455 | CL63 | HEK-293T | C2986(1.26); C2185(0.99); C447(0.94); C3023(0.93) | LDD1658 | [16] |
| LDCM0456 | CL64 | HEK-293T | C2986(0.90); C2185(0.93); C447(1.06); C3023(0.95) | LDD1659 | [16] |
| LDCM0457 | CL65 | HEK-293T | C2986(0.76); C2185(0.95); C447(1.03); C3023(0.96) | LDD1660 | [16] |
| LDCM0458 | CL66 | HEK-293T | C2986(0.91); C2185(1.03); C447(1.04); C3023(0.85) | LDD1661 | [16] |
| LDCM0459 | CL67 | HEK-293T | C2986(0.93); C2185(1.06); C447(1.04); C3023(0.90) | LDD1662 | [16] |
| LDCM0460 | CL68 | HEK-293T | C2986(0.95); C2185(1.00); C447(1.03); C3023(0.85) | LDD1663 | [16] |
| LDCM0461 | CL69 | HEK-293T | C2986(1.22); C2185(0.95); C447(1.01); C3023(0.90) | LDD1664 | [16] |
| LDCM0462 | CL7 | HEK-293T | C2986(0.89); C2185(0.89); C447(1.05); C3023(0.93) | LDD1665 | [16] |
| LDCM0463 | CL70 | HEK-293T | C2986(1.11); C2185(0.97); C447(1.10); C3023(1.04) | LDD1666 | [16] |
| LDCM0464 | CL71 | HEK-293T | C2185(1.00); C447(1.11); C3023(0.86); C2098(1.10) | LDD1667 | [16] |
| LDCM0465 | CL72 | HEK-293T | C2986(0.96); C2185(1.13); C447(1.02); C3023(0.93) | LDD1668 | [16] |
| LDCM0466 | CL73 | HEK-293T | C2986(0.82); C2185(0.93); C447(0.90); C3023(0.99) | LDD1669 | [16] |
| LDCM0467 | CL74 | HEK-293T | C2986(1.18); C2185(0.91); C447(1.00); C3023(0.87) | LDD1670 | [16] |
| LDCM0469 | CL76 | HEK-293T | C2986(0.95); C2185(0.90); C447(1.06); C3023(1.01) | LDD1672 | [16] |
| LDCM0470 | CL77 | HEK-293T | C2986(1.22); C2185(0.96); C447(1.03); C3023(1.16) | LDD1673 | [16] |
| LDCM0471 | CL78 | HEK-293T | C2986(0.98); C2185(0.96); C447(1.01); C3023(0.92) | LDD1674 | [16] |
| LDCM0472 | CL79 | HEK-293T | C2986(0.81); C2185(0.99); C447(1.00); C3023(0.90) | LDD1675 | [16] |
| LDCM0473 | CL8 | HEK-293T | C2986(1.58); C2185(0.85); C447(0.90); C3023(1.33) | LDD1676 | [16] |
| LDCM0474 | CL80 | HEK-293T | C2986(0.91); C2185(1.03); C447(0.96); C3023(0.90) | LDD1677 | [16] |
| LDCM0475 | CL81 | HEK-293T | C2986(1.05); C2185(0.95); C447(1.04); C3023(1.00) | LDD1678 | [16] |
| LDCM0476 | CL82 | HEK-293T | C2986(0.73); C2185(0.89); C447(1.07); C3023(1.00) | LDD1679 | [16] |
| LDCM0477 | CL83 | HEK-293T | C2185(0.94); C447(0.99); C3023(0.93); C2098(1.07) | LDD1680 | [16] |
| LDCM0478 | CL84 | HEK-293T | C2986(1.13); C2185(0.94); C447(1.04); C3023(0.97) | LDD1681 | [16] |
| LDCM0479 | CL85 | HEK-293T | C2986(0.75); C2185(0.97); C447(0.92); C3023(0.94) | LDD1682 | [16] |
| LDCM0480 | CL86 | HEK-293T | C2986(1.07); C2185(0.93); C447(0.95); C3023(0.92) | LDD1683 | [16] |
| LDCM0481 | CL87 | HEK-293T | C2986(1.44); C2185(1.07); C447(0.93); C3023(0.97) | LDD1684 | [16] |
| LDCM0482 | CL88 | HEK-293T | C2986(0.85); C2185(1.12); C447(0.95); C3023(0.87) | LDD1685 | [16] |
| LDCM0483 | CL89 | HEK-293T | C2986(1.12); C2185(0.91); C447(0.97); C3023(1.02) | LDD1686 | [16] |
| LDCM0484 | CL9 | HEK-293T | C2986(1.13); C2185(1.00); C447(0.92); C3023(0.99) | LDD1687 | [16] |
| LDCM0485 | CL90 | HEK-293T | C2986(1.40); C2185(0.88); C447(0.87); C3023(1.27) | LDD1688 | [16] |
| LDCM0486 | CL91 | HEK-293T | C2986(0.86); C2185(0.92); C447(0.97); C3023(0.89) | LDD1689 | [16] |
| LDCM0487 | CL92 | HEK-293T | C2986(1.02); C2185(1.01); C447(0.95); C3023(0.90) | LDD1690 | [16] |
| LDCM0488 | CL93 | HEK-293T | C2986(1.07); C2185(0.98); C447(0.95); C3023(0.98) | LDD1691 | [16] |
| LDCM0489 | CL94 | HEK-293T | C2986(0.83); C2185(0.97); C447(1.10); C3023(0.96) | LDD1692 | [16] |
| LDCM0490 | CL95 | HEK-293T | C2185(0.93); C447(1.11); C3023(1.22); C2098(0.92) | LDD1693 | [16] |
| LDCM0491 | CL96 | HEK-293T | C2986(0.83); C2185(1.02); C447(1.08); C3023(0.91) | LDD1694 | [16] |
| LDCM0492 | CL97 | HEK-293T | C2986(0.75); C2185(0.95); C447(0.98); C3023(1.03) | LDD1695 | [16] |
| LDCM0493 | CL98 | HEK-293T | C2986(1.17); C2185(0.94); C447(1.01); C3023(1.03) | LDD1696 | [16] |
| LDCM0494 | CL99 | HEK-293T | C2986(0.89); C2185(0.88); C447(0.97); C3023(0.93) | LDD1697 | [16] |
| LDCM0495 | E2913 | HEK-293T | C2986(0.86); C2185(0.88); C447(0.96); C3023(1.00) | LDD1698 | [16] |
| LDCM0213 | Electrophilic fragment 2 | MDA-MB-231 | C3023(2.40); C3076(1.40); C1627(0.99) | LDD1702 | [4] |
| LDCM0468 | Fragment33 | HEK-293T | C2986(1.25); C2185(0.96); C447(0.94); C3023(1.04) | LDD1671 | [16] |
| LDCM0427 | Fragment51 | HEK-293T | C2986(1.54); C2185(0.97); C447(0.97); C3023(0.97) | LDD1631 | [16] |
| LDCM0116 | HHS-0101 | DM93 | Y221(1.27) | LDD0264 | [6] |
| LDCM0117 | HHS-0201 | DM93 | Y221(4.62) | LDD0265 | [6] |
| LDCM0119 | HHS-0401 | DM93 | Y221(3.40) | LDD0267 | [6] |
| LDCM0120 | HHS-0701 | DM93 | Y221(4.09) | LDD0268 | [6] |
| LDCM0022 | KB02 | HEK-293T | C2986(1.09); C2185(0.89); C447(0.93); C3023(0.91) | LDD1492 | [16] |
| LDCM0023 | KB03 | HEK-293T | C2986(0.97); C2185(0.95); C447(1.01); C3023(1.03) | LDD1497 | [16] |
| LDCM0024 | KB05 | COLO792 | C99(1.69); C990(2.04); C2103(1.44) | LDD3310 | [3] |
| LDCM0528 | N-(4-bromophenyl)-2-cyano-N-phenylacetamide | MDA-MB-231 | C3023(0.74) | LDD2121 | [4] |
| LDCM0109 | NEM | HeLa | N.A. | LDD0223 | [7] |
| LDCM0496 | Nucleophilic fragment 11a | MDA-MB-231 | C3023(0.71) | LDD2089 | [4] |
| LDCM0499 | Nucleophilic fragment 12b | MDA-MB-231 | C1970(1.27) | LDD2092 | [4] |
| LDCM0500 | Nucleophilic fragment 13a | MDA-MB-231 | C1970(1.92) | LDD2093 | [4] |
| LDCM0501 | Nucleophilic fragment 13b | MDA-MB-231 | C1970(2.06) | LDD2094 | [4] |
| LDCM0503 | Nucleophilic fragment 14b | MDA-MB-231 | C3023(0.54) | LDD2096 | [4] |
| LDCM0505 | Nucleophilic fragment 15b | MDA-MB-231 | C3023(1.11); C1970(1.01) | LDD2098 | [4] |
| LDCM0506 | Nucleophilic fragment 16a | MDA-MB-231 | C1970(1.18) | LDD2099 | [4] |
| LDCM0512 | Nucleophilic fragment 19a | MDA-MB-231 | C1970(1.74) | LDD2105 | [4] |
| LDCM0514 | Nucleophilic fragment 20a | MDA-MB-231 | C1970(1.12) | LDD2107 | [4] |
| LDCM0516 | Nucleophilic fragment 21a | MDA-MB-231 | C1970(1.09) | LDD2109 | [4] |
| LDCM0523 | Nucleophilic fragment 24b | MDA-MB-231 | C1970(1.10) | LDD2116 | [4] |
| LDCM0525 | Nucleophilic fragment 25b | MDA-MB-231 | C2185(0.94) | LDD2118 | [4] |
| LDCM0527 | Nucleophilic fragment 26b | MDA-MB-231 | C3023(0.68) | LDD2120 | [4] |
| LDCM0530 | Nucleophilic fragment 28a | MDA-MB-231 | C1970(1.21) | LDD2123 | [4] |
| LDCM0532 | Nucleophilic fragment 29a | MDA-MB-231 | C1970(0.96) | LDD2125 | [4] |
| LDCM0533 | Nucleophilic fragment 29b | MDA-MB-231 | C2185(0.89) | LDD2126 | [4] |
| LDCM0534 | Nucleophilic fragment 30a | MDA-MB-231 | C1970(1.24) | LDD2127 | [4] |
| LDCM0535 | Nucleophilic fragment 30b | MDA-MB-231 | C3023(0.55) | LDD2128 | [4] |
| LDCM0536 | Nucleophilic fragment 31 | MDA-MB-231 | C1970(2.03) | LDD2129 | [4] |
| LDCM0543 | Nucleophilic fragment 38 | MDA-MB-231 | C1970(1.20) | LDD2136 | [4] |
| LDCM0544 | Nucleophilic fragment 39 | MDA-MB-231 | C1970(1.00) | LDD2137 | [4] |
| LDCM0546 | Nucleophilic fragment 40 | MDA-MB-231 | C1970(1.01) | LDD2140 | [4] |
| LDCM0547 | Nucleophilic fragment 41 | MDA-MB-231 | C3023(0.67) | LDD2141 | [4] |
| LDCM0549 | Nucleophilic fragment 43 | MDA-MB-231 | C3023(0.62) | LDD2143 | [4] |
| LDCM0550 | Nucleophilic fragment 5a | MDA-MB-231 | C1970(0.95); C514(1.64) | LDD2144 | [4] |
| LDCM0552 | Nucleophilic fragment 6a | MDA-MB-231 | C1970(1.18) | LDD2146 | [4] |
| LDCM0556 | Nucleophilic fragment 8a | MDA-MB-231 | C3023(0.53) | LDD2150 | [4] |
| LDCM0557 | Nucleophilic fragment 8b | MDA-MB-231 | C1970(0.97) | LDD2151 | [4] |
| LDCM0112 | W16 | Hep-G2 | C447(0.54) | LDD0239 | [14] |
The Interaction Atlas With This Target
References
