Details of the Target
General Information of Target
| Target ID | LDTP07458 | |||||
|---|---|---|---|---|---|---|
| Target Name | RPA-related protein RADX (RADX) | |||||
| Gene Name | RADX | |||||
| Gene ID | 55086 | |||||
| Synonyms |
CXorf57; RPA-related protein RADX; RPA-related and RAD51-antagonist, X-chromosome |
|||||
| 3D Structure | ||||||
| Sequence |
MSGESGQPEAGPSHAGLDWPNPERNRAGVPGGVIRRAGSQGPRSWIQKVLEQIMDSPRQC
VTPSEVVPVTVLAVQRYLLEDEPRDTVPKPPLYCYDVTISDGVYQEKCYLDPSLNSLVYQ NILKVGIQMRISRVSCLYNEKRIGQGILCIDNVHCGETSDSISLETPFRNRAHQEKPERP LRGGKSHYLALWNNEDPYGDIWLTDKQPEEHNFSDTKIISLSHLEMTWTNRRNFPALLVR ILHKSKLRYYGKPDKKMIEPYQTFLEVADSSGTVSVIMWNALCPEWYKSLRVGLVLLLQD YSVKKSYPFRIQPVPVDPQIKLISTMEICLNLRDPPTNIIIIPEKQVKPEWRLPKLNHRF TTRSELDDMPENCICDVIGLLVFVGRVQRSKKKENREDFWSYRWIHIADGTSEQPFIVEL FSTSQPEIFENIYPMAYFVCTQLKVVRNDNQVPKLLYLTTTNESGVFITGHRGQPYTYDA KVKNFIQWIRTKSDSGEQKNMVIGGYYPYPPVPETFSKYSSSIKVESLLTAISEVRKEIE DLQYREQKRIAIQGIITAIKYIPHSSATESASASETLRNANRPSTSQAARVEIQERNGKR HQDDEPVNSQYFQTTSTNLSLSNKIRILQGPHANPVAVPQPGASVQTKGIKPGMPSIFNR RANINANLQGKARKTISDRWESQLWREKKFGLIDHLHYSRVYPESIPRKFMFEHRKFLSD QYNSQPAKYVPPEGRPPKLDDFKSARSLGHFEVTILGLNHEIAIDVAFLPMYCPEDIRTS QIDTLLTSMNYSCAYPQDTTGNDRLPGPRAVAGDIIKAATELDRVHIVGILDICNLGNNK VEVYLHKIYSPENTS |
|||||
| Target Bioclass |
Other
|
|||||
| Subcellular location |
Chromosome
|
|||||
| Function |
Single-stranded DNA-binding protein recruited to replication forks to maintain genome stability. Prevents fork collapse by antagonizing the accumulation of RAD51 at forks to ensure the proper balance of fork remodeling and protection without interfering with the capacity of cells to complete homologous recombination of double-strand breaks.
|
|||||
| Uniprot ID | ||||||
| Ensemble ID | ||||||
| HGNC ID | ||||||
Target Site Mutations in Different Cell Lines
| Cell line | Mutation details | Probe for labeling this protein in this cell | |||
|---|---|---|---|---|---|
| COLO320 | SNV: p.A571T | DBIA Probe Info | |||
| HKGZCC | SNV: p.F710L | . | |||
| Ishikawa (Heraklio) 02 ER | SNV: p.S412L | . | |||
| KYSE150 | SNV: p.F168Y | . | |||
| LS180 | SNV: p.K252N | DBIA Probe Info | |||
| MELJUSO | SNV: p.E266D | DBIA Probe Info | |||
| NCIH2172 | SNV: p.P641L | . | |||
| NCIH23 | SNV: p.I320F | . | |||
| OCIAML2 | SNV: p.I532T | . | |||
| SNGM | SNV: p.Y198C | . | |||
Probe(s) Labeling This Target
ABPP Probe
| Probe name | Structure | Binding Site(Ratio) | Interaction ID | Ref | |
|---|---|---|---|---|---|
|
DBIA Probe Info |
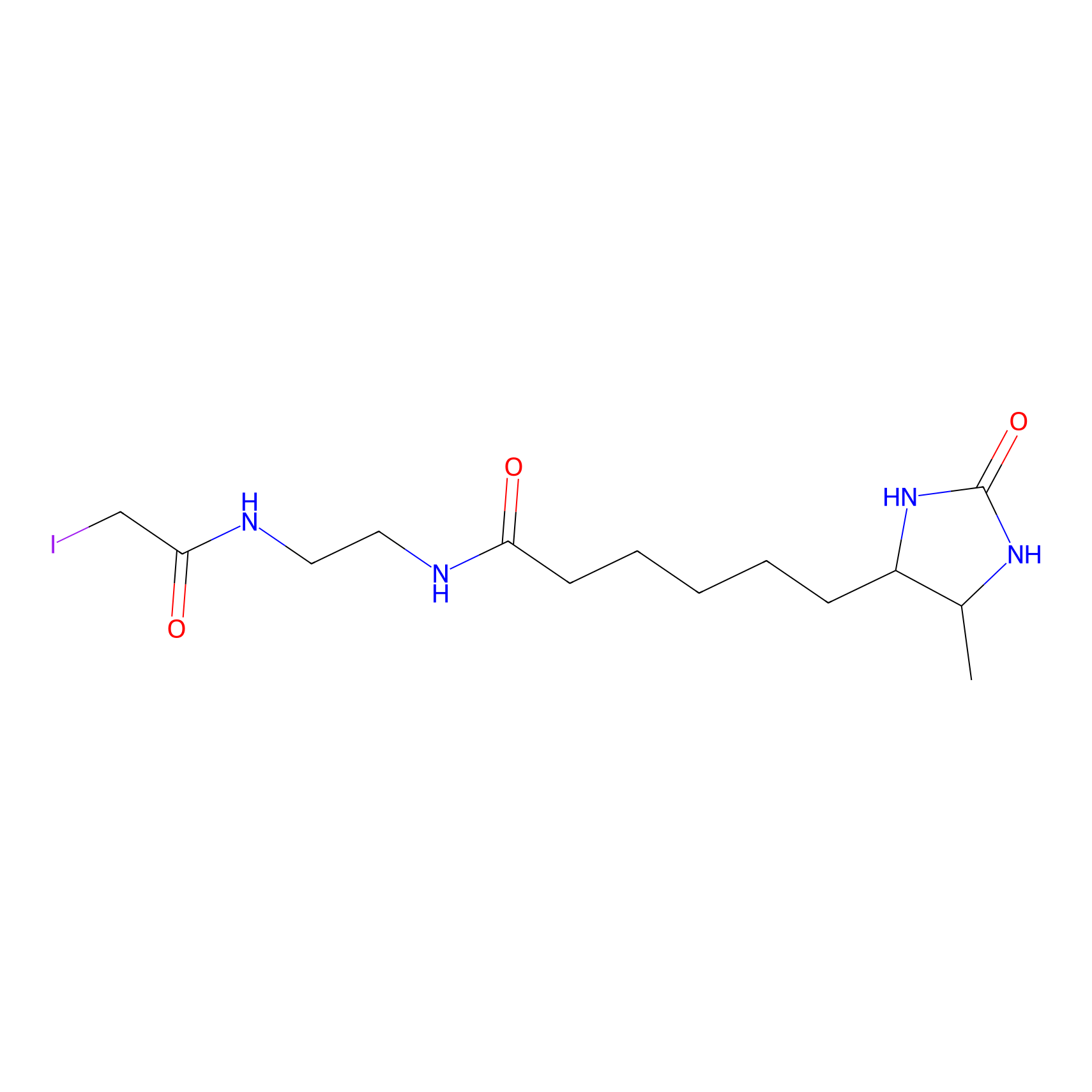 |
C793(2.76); C108(2.75) | LDD0080 | [1] | |
|
IA-alkyne Probe Info |
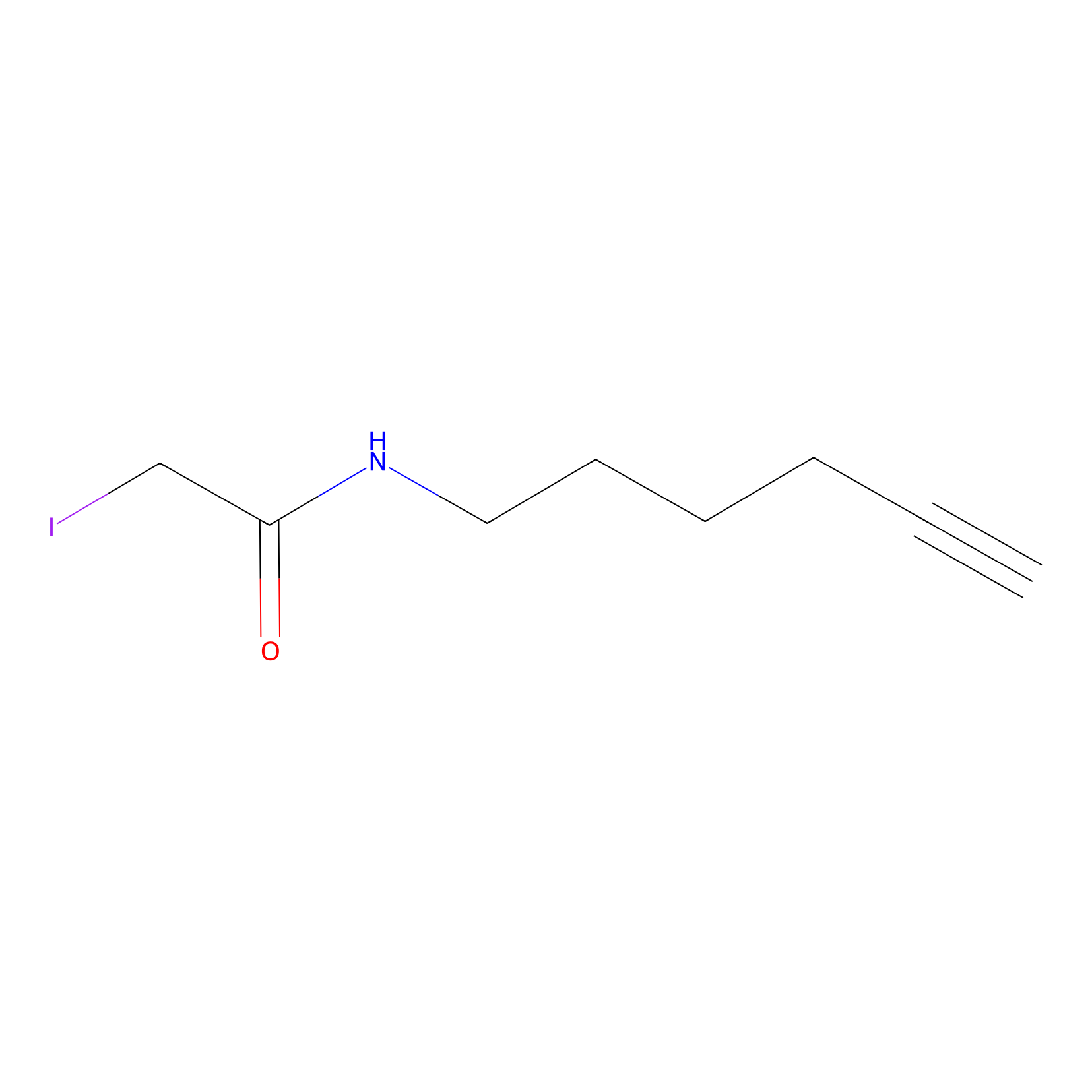 |
C149(0.00); C793(0.00) | LDD0165 | [2] | |
|
IPM Probe Info |
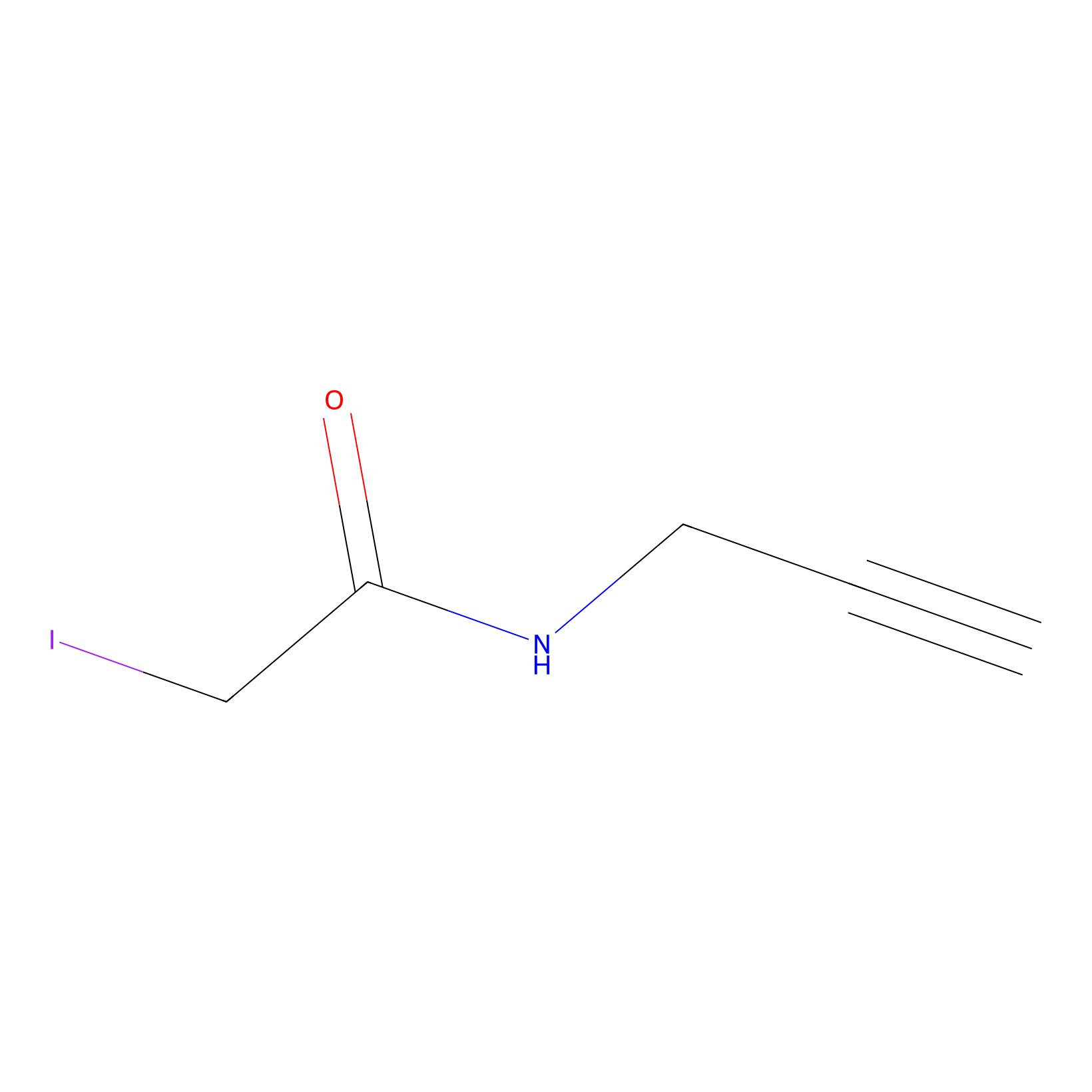 |
C60(0.00); C283(0.00); C136(0.00); C108(0.00) | LDD2156 | [3] | |
|
AOyne Probe Info |
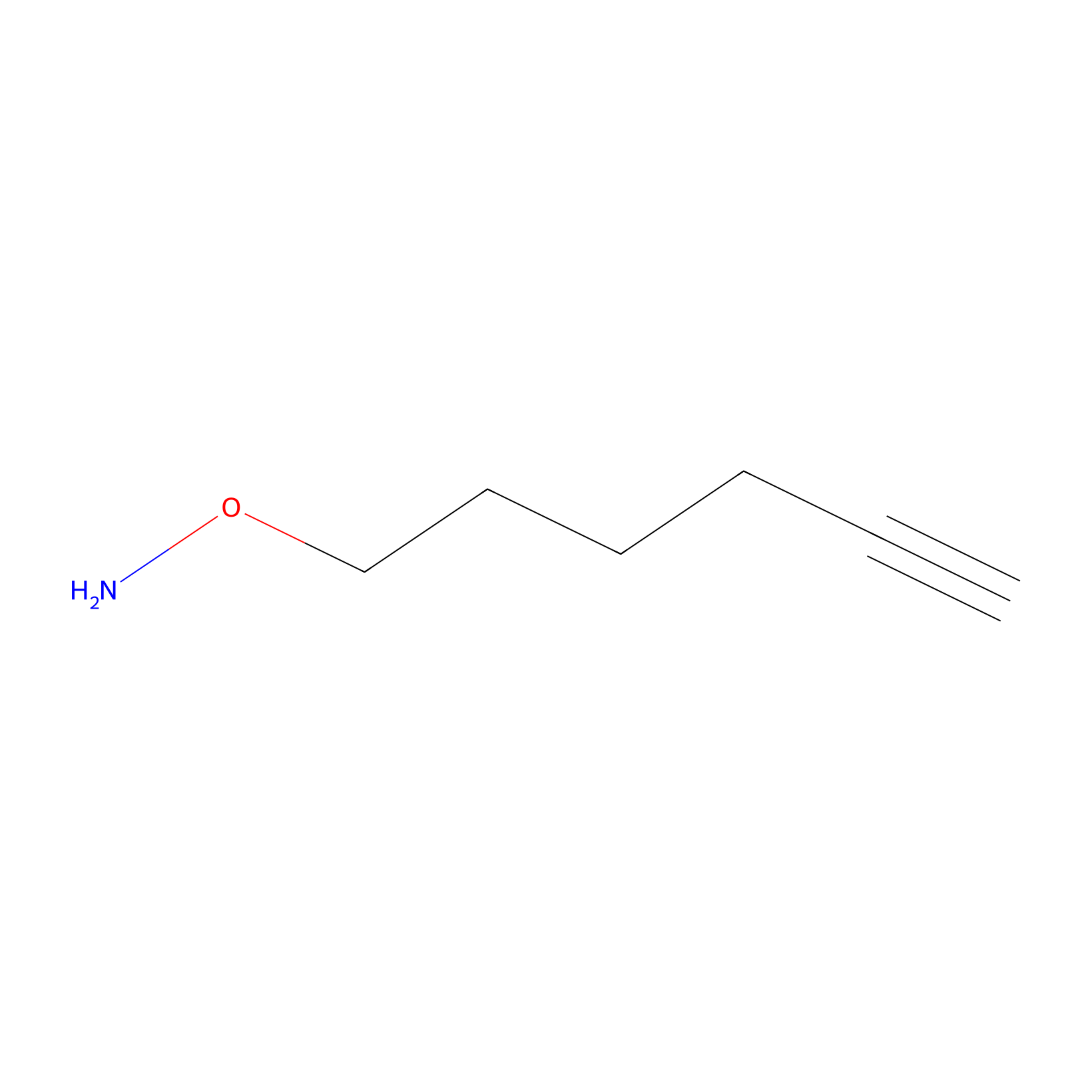 |
13.40 | LDD0443 | [4] | |
Competitor(s) Related to This Target
| Competitor ID | Name | Cell line | Binding Site(Ratio) | Interaction ID | Ref |
|---|---|---|---|---|---|
| LDCM0214 | AC1 | HEK-293T | C136(0.91); C329(1.02) | LDD1507 | [5] |
| LDCM0215 | AC10 | HEK-293T | C136(0.85); C329(1.00) | LDD1508 | [5] |
| LDCM0226 | AC11 | HEK-293T | C136(1.02) | LDD1509 | [5] |
| LDCM0259 | AC14 | HEK-293T | C136(1.07) | LDD1512 | [5] |
| LDCM0270 | AC15 | HEK-293T | C136(1.00) | LDD1513 | [5] |
| LDCM0276 | AC17 | HEK-293T | C136(0.95); C329(1.16) | LDD1515 | [5] |
| LDCM0277 | AC18 | HEK-293T | C136(1.00); C329(0.74) | LDD1516 | [5] |
| LDCM0278 | AC19 | HEK-293T | C136(0.92) | LDD1517 | [5] |
| LDCM0279 | AC2 | HEK-293T | C136(0.92); C329(1.61) | LDD1518 | [5] |
| LDCM0282 | AC22 | HEK-293T | C136(1.16) | LDD1521 | [5] |
| LDCM0283 | AC23 | HEK-293T | C136(1.00) | LDD1522 | [5] |
| LDCM0284 | AC24 | HEK-293T | C136(1.03) | LDD1523 | [5] |
| LDCM0285 | AC25 | HEK-293T | C136(1.00); C329(1.11) | LDD1524 | [5] |
| LDCM0286 | AC26 | HEK-293T | C136(0.90); C329(0.73) | LDD1525 | [5] |
| LDCM0287 | AC27 | HEK-293T | C136(0.95) | LDD1526 | [5] |
| LDCM0290 | AC3 | HEK-293T | C136(1.01) | LDD1529 | [5] |
| LDCM0291 | AC30 | HEK-293T | C136(0.99) | LDD1530 | [5] |
| LDCM0292 | AC31 | HEK-293T | C136(0.99) | LDD1531 | [5] |
| LDCM0293 | AC32 | HEK-293T | C136(1.05) | LDD1532 | [5] |
| LDCM0294 | AC33 | HEK-293T | C136(1.27); C329(1.28) | LDD1533 | [5] |
| LDCM0295 | AC34 | HEK-293T | C136(0.97); C329(0.75) | LDD1534 | [5] |
| LDCM0296 | AC35 | HEK-293T | C136(0.99) | LDD1535 | [5] |
| LDCM0299 | AC38 | HEK-293T | C136(1.01) | LDD1538 | [5] |
| LDCM0300 | AC39 | HEK-293T | C136(0.94) | LDD1539 | [5] |
| LDCM0302 | AC40 | HEK-293T | C136(1.06) | LDD1541 | [5] |
| LDCM0303 | AC41 | HEK-293T | C136(1.05); C329(1.25) | LDD1542 | [5] |
| LDCM0304 | AC42 | HEK-293T | C136(0.85); C329(0.73) | LDD1543 | [5] |
| LDCM0305 | AC43 | HEK-293T | C136(0.99) | LDD1544 | [5] |
| LDCM0308 | AC46 | HEK-293T | C136(1.06) | LDD1547 | [5] |
| LDCM0309 | AC47 | HEK-293T | C136(1.01) | LDD1548 | [5] |
| LDCM0310 | AC48 | HEK-293T | C136(0.89) | LDD1549 | [5] |
| LDCM0311 | AC49 | HEK-293T | C136(1.05); C329(1.16) | LDD1550 | [5] |
| LDCM0313 | AC50 | HEK-293T | C136(0.89); C329(0.89) | LDD1552 | [5] |
| LDCM0314 | AC51 | HEK-293T | C136(1.03) | LDD1553 | [5] |
| LDCM0317 | AC54 | HEK-293T | C136(1.06) | LDD1556 | [5] |
| LDCM0318 | AC55 | HEK-293T | C136(1.01) | LDD1557 | [5] |
| LDCM0319 | AC56 | HEK-293T | C136(1.03) | LDD1558 | [5] |
| LDCM0320 | AC57 | HEK-293T | C136(0.79); C329(1.03) | LDD1559 | [5] |
| LDCM0321 | AC58 | HEK-293T | C136(0.92); C329(1.23) | LDD1560 | [5] |
| LDCM0322 | AC59 | HEK-293T | C136(0.96) | LDD1561 | [5] |
| LDCM0323 | AC6 | HEK-293T | C136(0.93) | LDD1562 | [5] |
| LDCM0326 | AC62 | HEK-293T | C136(1.15) | LDD1565 | [5] |
| LDCM0327 | AC63 | HEK-293T | C136(0.96) | LDD1566 | [5] |
| LDCM0328 | AC64 | HEK-293T | C136(1.01) | LDD1567 | [5] |
| LDCM0334 | AC7 | HEK-293T | C136(0.99) | LDD1568 | [5] |
| LDCM0345 | AC8 | HEK-293T | C136(1.04) | LDD1569 | [5] |
| LDCM0356 | AKOS034007680 | HEK-293T | C136(0.92); C329(1.01) | LDD1570 | [5] |
| LDCM0275 | AKOS034007705 | HEK-293T | C136(1.12) | LDD1514 | [5] |
| LDCM0368 | CL10 | HEK-293T | C136(1.19) | LDD1572 | [5] |
| LDCM0371 | CL102 | HEK-293T | C136(1.17) | LDD1575 | [5] |
| LDCM0375 | CL106 | HEK-293T | C136(0.96) | LDD1579 | [5] |
| LDCM0379 | CL11 | HEK-293T | C136(1.13) | LDD1583 | [5] |
| LDCM0380 | CL110 | HEK-293T | C136(0.84) | LDD1584 | [5] |
| LDCM0384 | CL114 | HEK-293T | C136(0.90) | LDD1588 | [5] |
| LDCM0388 | CL118 | HEK-293T | C136(1.16) | LDD1592 | [5] |
| LDCM0390 | CL12 | HEK-293T | C136(1.20) | LDD1594 | [5] |
| LDCM0393 | CL122 | HEK-293T | C136(1.08) | LDD1597 | [5] |
| LDCM0397 | CL126 | HEK-293T | C136(1.01) | LDD1601 | [5] |
| LDCM0401 | CL14 | HEK-293T | C136(1.11) | LDD1605 | [5] |
| LDCM0404 | CL17 | HEK-293T | C136(0.94); C329(1.05) | LDD1608 | [5] |
| LDCM0405 | CL18 | HEK-293T | C136(0.88); C329(1.01) | LDD1609 | [5] |
| LDCM0406 | CL19 | HEK-293T | C136(1.08) | LDD1610 | [5] |
| LDCM0407 | CL2 | HEK-293T | C136(1.00) | LDD1611 | [5] |
| LDCM0410 | CL22 | HEK-293T | C136(1.00) | LDD1614 | [5] |
| LDCM0411 | CL23 | HEK-293T | C136(1.10) | LDD1615 | [5] |
| LDCM0412 | CL24 | HEK-293T | C136(1.25) | LDD1616 | [5] |
| LDCM0414 | CL26 | HEK-293T | C136(0.88) | LDD1618 | [5] |
| LDCM0417 | CL29 | HEK-293T | C136(0.78); C329(0.92) | LDD1621 | [5] |
| LDCM0419 | CL30 | HEK-293T | C136(0.96); C329(1.20) | LDD1623 | [5] |
| LDCM0420 | CL31 | HEK-293T | C136(1.11) | LDD1624 | [5] |
| LDCM0423 | CL34 | HEK-293T | C136(1.03) | LDD1627 | [5] |
| LDCM0424 | CL35 | HEK-293T | C136(1.11) | LDD1628 | [5] |
| LDCM0425 | CL36 | HEK-293T | C136(1.23) | LDD1629 | [5] |
| LDCM0431 | CL41 | HEK-293T | C136(0.75); C329(1.04) | LDD1635 | [5] |
| LDCM0432 | CL42 | HEK-293T | C136(0.97); C329(0.99) | LDD1636 | [5] |
| LDCM0433 | CL43 | HEK-293T | C136(1.01) | LDD1637 | [5] |
| LDCM0436 | CL46 | HEK-293T | C136(1.02) | LDD1640 | [5] |
| LDCM0437 | CL47 | HEK-293T | C136(1.11) | LDD1641 | [5] |
| LDCM0438 | CL48 | HEK-293T | C136(0.89) | LDD1642 | [5] |
| LDCM0440 | CL5 | HEK-293T | C136(0.97); C329(1.01) | LDD1644 | [5] |
| LDCM0441 | CL50 | HEK-293T | C136(1.01) | LDD1645 | [5] |
| LDCM0444 | CL53 | HEK-293T | C136(0.81); C329(0.80) | LDD1647 | [5] |
| LDCM0445 | CL54 | HEK-293T | C136(0.90); C329(0.71) | LDD1648 | [5] |
| LDCM0446 | CL55 | HEK-293T | C136(1.03) | LDD1649 | [5] |
| LDCM0449 | CL58 | HEK-293T | C136(1.01) | LDD1652 | [5] |
| LDCM0450 | CL59 | HEK-293T | C136(1.02) | LDD1653 | [5] |
| LDCM0451 | CL6 | HEK-293T | C136(0.95); C329(0.63) | LDD1654 | [5] |
| LDCM0452 | CL60 | HEK-293T | C136(0.93) | LDD1655 | [5] |
| LDCM0454 | CL62 | HEK-293T | C136(1.02) | LDD1657 | [5] |
| LDCM0457 | CL65 | HEK-293T | C136(1.04); C329(1.02) | LDD1660 | [5] |
| LDCM0458 | CL66 | HEK-293T | C136(0.88); C329(1.01) | LDD1661 | [5] |
| LDCM0459 | CL67 | HEK-293T | C136(0.96) | LDD1662 | [5] |
| LDCM0462 | CL7 | HEK-293T | C136(1.12) | LDD1665 | [5] |
| LDCM0463 | CL70 | HEK-293T | C136(1.33) | LDD1666 | [5] |
| LDCM0464 | CL71 | HEK-293T | C136(0.98) | LDD1667 | [5] |
| LDCM0465 | CL72 | HEK-293T | C136(1.02) | LDD1668 | [5] |
| LDCM0467 | CL74 | HEK-293T | C136(0.73) | LDD1670 | [5] |
| LDCM0470 | CL77 | HEK-293T | C136(1.17); C329(0.92) | LDD1673 | [5] |
| LDCM0471 | CL78 | HEK-293T | C136(0.89); C329(0.73) | LDD1674 | [5] |
| LDCM0472 | CL79 | HEK-293T | C136(0.98) | LDD1675 | [5] |
| LDCM0476 | CL82 | HEK-293T | C136(1.03) | LDD1679 | [5] |
| LDCM0477 | CL83 | HEK-293T | C136(1.00) | LDD1680 | [5] |
| LDCM0478 | CL84 | HEK-293T | C136(1.07) | LDD1681 | [5] |
| LDCM0480 | CL86 | HEK-293T | C136(1.14) | LDD1683 | [5] |
| LDCM0483 | CL89 | HEK-293T | C136(1.00); C329(1.05) | LDD1686 | [5] |
| LDCM0485 | CL90 | HEK-293T | C136(1.01); C329(0.75) | LDD1688 | [5] |
| LDCM0486 | CL91 | HEK-293T | C136(1.03) | LDD1689 | [5] |
| LDCM0489 | CL94 | HEK-293T | C136(1.12) | LDD1692 | [5] |
| LDCM0490 | CL95 | HEK-293T | C136(1.06) | LDD1693 | [5] |
| LDCM0491 | CL96 | HEK-293T | C136(1.06) | LDD1694 | [5] |
| LDCM0493 | CL98 | HEK-293T | C136(0.91) | LDD1696 | [5] |
| LDCM0427 | Fragment51 | HEK-293T | C136(1.00) | LDD1631 | [5] |
| LDCM0022 | KB02 | HCT 116 | C793(2.76); C108(2.75) | LDD0080 | [1] |
| LDCM0023 | KB03 | HCT 116 | C793(2.61); C108(4.65) | LDD0081 | [1] |
| LDCM0024 | KB05 | HCT 116 | C793(3.60); C108(3.12) | LDD0082 | [1] |
The Interaction Atlas With This Target
References
